WO2013147320A1 - βグロビン遺伝子の変異を検出するためのマイクロアレイ及びその検出方法 - Google Patents
βグロビン遺伝子の変異を検出するためのマイクロアレイ及びその検出方法 Download PDFInfo
- Publication number
- WO2013147320A1 WO2013147320A1 PCT/JP2013/060261 JP2013060261W WO2013147320A1 WO 2013147320 A1 WO2013147320 A1 WO 2013147320A1 JP 2013060261 W JP2013060261 W JP 2013060261W WO 2013147320 A1 WO2013147320 A1 WO 2013147320A1
- Authority
- WO
- WIPO (PCT)
- Prior art keywords
- probe
- polymorphism
- sequence
- straight line
- detection
- Prior art date
Links
Images
Classifications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6876—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes
- C12Q1/6883—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes for diseases caused by alterations of genetic material
-
- G—PHYSICS
- G16—INFORMATION AND COMMUNICATION TECHNOLOGY [ICT] SPECIALLY ADAPTED FOR SPECIFIC APPLICATION FIELDS
- G16B—BIOINFORMATICS, i.e. INFORMATION AND COMMUNICATION TECHNOLOGY [ICT] SPECIALLY ADAPTED FOR GENETIC OR PROTEIN-RELATED DATA PROCESSING IN COMPUTATIONAL MOLECULAR BIOLOGY
- G16B25/00—ICT specially adapted for hybridisation; ICT specially adapted for gene or protein expression
- G16B25/20—Polymerase chain reaction [PCR]; Primer or probe design; Probe optimisation
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6876—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes
-
- G—PHYSICS
- G01—MEASURING; TESTING
- G01N—INVESTIGATING OR ANALYSING MATERIALS BY DETERMINING THEIR CHEMICAL OR PHYSICAL PROPERTIES
- G01N21/00—Investigating or analysing materials by the use of optical means, i.e. using sub-millimetre waves, infrared, visible or ultraviolet light
- G01N21/62—Systems in which the material investigated is excited whereby it emits light or causes a change in wavelength of the incident light
- G01N21/63—Systems in which the material investigated is excited whereby it emits light or causes a change in wavelength of the incident light optically excited
- G01N21/64—Fluorescence; Phosphorescence
- G01N21/6428—Measuring fluorescence of fluorescent products of reactions or of fluorochrome labelled reactive substances, e.g. measuring quenching effects, using measuring "optrodes"
-
- G—PHYSICS
- G16—INFORMATION AND COMMUNICATION TECHNOLOGY [ICT] SPECIALLY ADAPTED FOR SPECIFIC APPLICATION FIELDS
- G16B—BIOINFORMATICS, i.e. INFORMATION AND COMMUNICATION TECHNOLOGY [ICT] SPECIALLY ADAPTED FOR GENETIC OR PROTEIN-RELATED DATA PROCESSING IN COMPUTATIONAL MOLECULAR BIOLOGY
- G16B25/00—ICT specially adapted for hybridisation; ICT specially adapted for gene or protein expression
-
- G—PHYSICS
- G16—INFORMATION AND COMMUNICATION TECHNOLOGY [ICT] SPECIALLY ADAPTED FOR SPECIFIC APPLICATION FIELDS
- G16B—BIOINFORMATICS, i.e. INFORMATION AND COMMUNICATION TECHNOLOGY [ICT] SPECIALLY ADAPTED FOR GENETIC OR PROTEIN-RELATED DATA PROCESSING IN COMPUTATIONAL MOLECULAR BIOLOGY
- G16B30/00—ICT specially adapted for sequence analysis involving nucleotides or amino acids
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q2600/00—Oligonucleotides characterized by their use
- C12Q2600/156—Polymorphic or mutational markers
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q2600/00—Oligonucleotides characterized by their use
- C12Q2600/16—Primer sets for multiplex assays
-
- G—PHYSICS
- G01—MEASURING; TESTING
- G01N—INVESTIGATING OR ANALYSING MATERIALS BY DETERMINING THEIR CHEMICAL OR PHYSICAL PROPERTIES
- G01N21/00—Investigating or analysing materials by the use of optical means, i.e. using sub-millimetre waves, infrared, visible or ultraviolet light
- G01N21/62—Systems in which the material investigated is excited whereby it emits light or causes a change in wavelength of the incident light
- G01N21/63—Systems in which the material investigated is excited whereby it emits light or causes a change in wavelength of the incident light optically excited
- G01N21/64—Fluorescence; Phosphorescence
- G01N21/6428—Measuring fluorescence of fluorescent products of reactions or of fluorochrome labelled reactive substances, e.g. measuring quenching effects, using measuring "optrodes"
- G01N2021/6439—Measuring fluorescence of fluorescent products of reactions or of fluorochrome labelled reactive substances, e.g. measuring quenching effects, using measuring "optrodes" with indicators, stains, dyes, tags, labels, marks
Abstract
Description
一塩基多型(SNP)とは、DNAの塩基配列の中でたった1つの塩基の違うことであり、酒に強い弱いや、薬が効きやすいかどうかなど、人間の個性の最小単位にあたるものである。ヒトゲノム30億塩基対の内、一塩基多型(SNP)は約300万個(500~1000塩基対に1個の割合)~1000万個存在すると示唆され、特定のタンパク質が生成されなかったり、他人と違うものが生成されたりすることにより個人差(体質)、人種差などの違いをもたらしている。ヒトにおける遺伝子の個人差の研究では、一塩基多型を解析して、病気に対する感受性や薬物への応答を調べ、そのヒト個人にあった副作用の少ない薬を投薬するようなオーダーメイド医療が可能になると言われ、一塩基多型(SNP)の解析の研究が進められている。
一塩基多型(SNP)が注目を集める理由は、核酸解析技術の向上により多数のSNPの解析が可能となり、また疾患とSNPとの関連が明らかになってきたからである。疾患関連遺伝子や、薬剤代謝の個人差の解析及び慢性疾患など広範囲な領域でSNPとの関連が明らかになってきている。今後もSNPとこれらの関連が益々明らかになってくるものと期待されている。
核酸解析技術は、非常に多くの試料を取扱い、膨大な数の操作が含まれているが、複雑で時間がかかり、一般に高い精度が要求されるものである。核酸解析技術の内、多数の遺伝子変異を速やかに高い精度で検出する手段として、SNP検出用DNAチップ(DNAチップは、DNAマイクロアレイとも言う。以下特に断らない限り同義とする。)が有効であることが知られている。
DNAチップとは、核酸プローブ(プローブ)が担体のそれぞれ決まった区画に固定化されたものであり、通常、核酸プローブには、被検核酸断片に対して相補的な塩基配列を有する1本鎖のDNAあるいはオリゴヌクレオチド分子が用いられる。
SNP検出用DNAチップには、核酸プローブとして、変異核酸の検査対象部位に相当する核酸断片の相補鎖が固定されている。変異の検査対象部位には、通常、1つの正常型と複数の変異型が存在し、それらのいずれかにマッチングする核酸プローブがプロット内に配列される。被検試料は、変異した検査対象部位に相当する核酸断片のみをPCR法に代表される核酸増幅法により増幅させた検体液を用いる。
この検体液を、SNP検出用DNAチップの核酸プローブが固定された面に接触させ、検体核酸断片と対応する核酸プローブ間でハイブリダイゼーションを起こさせる。そして、このハイブリダイゼーションによる結合を光学的、あるいは、電気化学的なシグナルとして検出することにより、核酸プローブと結合した検体核酸断片を同定し、かつ、定量することができる。
ここで、核酸プローブと検体の組合せが、野生型プローブと野生型検体、あるいは、変異型プローブとそれに対応する変異型検体のようなパーフェクトマッチでは、ハイブリダイゼーションが完全であり強い結合となる。一方、核酸プローブと検体の組合せが、野生型プローブと変異型検体、あるいは、変異型プローブと野生型検体のようなミスマッチでは、水素結合の出来ない部位を必然的に伴うので、ハイブリダイゼーションが不完全であり、弱い結合となる。
通常、高い特異性を維持するために温度、塩、洗剤、溶媒、カオトロピック剤及び変性剤の種々の組合せにより達成される最も厳格な条件下でハイブリダイゼーションを行い、パーフェクトマッチとミスマッチとにおけるハイブリダイゼーションの結合力の差異に由来するシグナル強度の差異を検出することにより、検体中の遺伝子型を識別し、確定することが可能になる。
ところで、ヘモグロビンは、酸素を肺から細胞へそして二酸化炭素を細胞から肺へ運搬する鉄含有のアロステリック複合体タンパク質である。ヘモグロビンAは、主要な成熟ヘモグロビンタンパク質であり、4つのポリペプチド鎖(2つのα−グロビン鎖及び2つのβグロビン鎖)を含む。
多くのヒトの病気は、ヘモグロビンポリペプチド鎖をコードする1つ以上の遺伝子に影響を与える遺伝子変異に原因があるとされる。このような病気には鎌状赤血球貧血が含まれ、ヘモグロビンβ鎖中の点変異により生じる。また、βサラセミア症状は、1つの型のグロビン鎖の不十分な合成によって表現型で顕著になった遺伝子変異から生じる血液関連疾患であり、他の型のグロビン鎖の過剰合成を生じる(例えば、非特許文献1参照)。
一方、分子生物学的技法の最近の開発は、特定のヒトの病気の状態及び症状を引き起こす又は関連する遺伝子異常への研究を可能にしている。ポリメラーゼ連鎖反応(PCR)及びその多くの改変した手法は、病気の状態及び症状にある遺伝子異常の研究のための特に有用な道具となる(例えば、非特許文献2及び3参照)。
PCR法の使用は、特定の目的DNA又はそのDNAの部分を増幅し、増幅した部分のさらなる特徴付けを容易にする。このようなさらなる特徴付けには、サイズを決定するためのゲル電気泳動、ヌクレオチド配列決定、特定のプローブを使用するハイブリダイゼーション研究等が含まれる(例えば、非特許文献4参照)。
近年、SNPs(一塩基多型)等の遺伝子型(すなわち遺伝子多型)と疾病等との因果関係に関する研究が数多く行われ、遺伝子異常が特定の個体のゲノムに存在するか否かの決定が行われてきた。
SNPs等の一塩基変異又は2以上の塩基数の遺伝子変異を判定(検出)する方法としては、まずPCR‐SSP法がある。この手法は、変異した遺伝子の塩基配列に特異なプライマーを合成してPCRを実施することから、数十個の遺伝子変異を判別するためには数十対のプライマーが必要となる。
この方法は分析時間が短く簡便な方法であるが、そうしたプライマーを合成する際には細心な注意と知識及び時間が要求されるため、大量の検体分析には限界がある。加えて変異を検出したい箇所が多いほどPCR‐SSPの数も多くなるため、多数の検体を一度に扱うのは難しいという欠点がある。
第2の方法としては、古くから行われている制限酵素断片長多型法(PCR‐RFLP法)が考えられる。共通配列部位にプライマーを設定し、その内側、すなわち、PCR産物内に多型性をもたせて増幅する。増幅の後、増幅産物を様々な制限酵素によって切断し、そのDNA断片の大きさで遺伝子配列の変異を類別する。
この方法は結果の判定が易しく方法も簡単ではあるが、制限酵素が認識できる部位が限定された場合に判別が困難となり、また、検体の分離にはポリアクリルアミドゲルを使用しなければならないため、大量の検体や数十個の変異を同時に類別することは難しい。更に、一般に全血検体をそのままPCR増幅を行った後、制限酵素で断片化した場合、増幅検体中に全血由来のタンパクが残存し、制限酵素による切断が不完全になることが報告されている。つまり、DNAに結合したタンパク質がDNAから離れていないため、制限酵素がDNAに結合できずに切断反応が正常に進まず、DNA抽出操作の必要性が生じる。
第3の方法として、PCR‐SSCP法がある。当該方法は、PCR産物をホルムアミド等の変性剤を添加して一本鎖DNA(ssDNA)に変性させた後に、非変性ポリアクリルアミドゲルで電気泳動する方法である。電気泳動においてssDNAは、その塩基配列に基づく特有の構造を有し、電気泳動中に固有の移動速度を示してそれぞれ異なるタイプのバンドを形成する。
この方法は、塩基配列に基づいて固有の移動速度を示すという性質を利用して塩基配列中の変異を類別する方法であるが、複雑かつ難易度の高い技術が必要であり、その結果の解析にも経験と知識が必要とされる。
第4の方法としては、PCR−SSO(sequence specific oligonucleotide)法が考えられる。PCR−SSOは正常部位と変異部位に対する合成プローブをフィルターにドットされた(マイクロプレートを用いることもある)PCR産物とハイブリダイズさせて、変異の有無を検出する方法である。また、逆にプローブをドットし、PCR産物をハイブリダイズするリバースドットブロット法もある。抗原抗体反応に例えると、DNAが抗原で変異部位に対する特異的抗体と正常部位に特異的な抗体とを作用させて、何れの抗体と結合したかを観察する方法である。従来この方法の検出には、放射性同位元素が使用されていたが、使用施設の制約等から化学発光や発色等によって検出されるようになってきている。
本方法は簡便ではあるが、サンプル量を相当量確保するか、そうでない場合は逆に感度を向上させる手法を導入する必要がある(例えば、非特許文献5及び6、特許文献1参照)。
第5の方法としては、直接塩基配列決定法が知られている。直接塩基配列決定法は、PCR増幅したDNA鎖を鋳型として、ベクターにサブクローニング等をしたりすることなく、直接塩基配列を決定する方法である。
この方法は、PCR増幅したDNA鎖を非対称PCRと呼ばれる二次PCRを行ない一本鎖DNA増幅して、一般的にはジデオキシ法を用いて塩基配列を決定する。この二次PCRは、一組のプライマーの一方を制限量にして(通常は1:10~1:100)PCRを行なうことによって一本鎖DNAを増幅する。最近ではサイクルシーケンス法が応用されるようになり、より簡単にシーケンス反応が行えるようになってきている。しかしながら、キットの価格が非常に高く、高価な装置も必要であり、実験過程も複雑であるため多量の検体を解析していくためにはコストがかかる。
従って、本発明の主な目的は、簡便かつ短時間に多数の変異(検体)を検出することができる、βグロビン遺伝子の変異を検出するためのマイクロアレイを提供することにある。
本発明者らは、従来技術の問題点に鑑みて鋭意検討を重ねた結果、特定の配列を有するプローブを複数種類使用することにより上記目的を達成できることを見出し、本発明を完成するに至った。
すなわち、本発明は、配列番号3、4、7、8、11、12、17、18と配列番号25~66に示される遺伝子を含むβグロビン遺伝子の変異を検出するためのプローブ群、当該プローブ群が固定化されたマイクロアレイ、当該マイクロアレイを用いた変異の検出方法及びキットに関する。
本発明によれば、PCR産物を精製することなく、ハイブリダイゼーション溶液を混合して直接マイクロアレイに接触・反応させることができるため、多量の検体を用いた場合においても短時間で処理を進めることができる。さらには、βグロビン遺伝子の変異25箇所を一度に検出することができるため、実用性、有用性に優れたものである。
以下、本発明を詳細に説明する。以下の実施の形態は、本発明を説明するための例示であり、本発明をこの実施の形態のみに限定する趣旨ではない。本発明は、その要旨を逸脱しない限り、様々な形態で実施をすることができる。
なお、本明細書において引用した全ての文献、および公開公報、特許公報その他の特許文献は、参照として本明細書に組み込むものとする。また、本明細書は、本願優先権主張の基礎となる2012年03月29日に出願された日本国特許出願(特願2012−077394号)の明細書及び図面に記載の内容を包含する。
以下、本発明を詳細に説明する。以下の実施の形態は、本発明を説明するための例示であり、本発明をこの実施の形態のみに限定する趣旨ではない。本発明は、その要旨を逸脱しない限り、様々な形態で実施をすることができる。
また、特に記載のない場合、アミノ酸配列は左端をアミノ末端及び右端をカルボキシル末端とし、塩基配列は左端を5’末端及び右端を3’末端として表わすものとする。
1.多型検出用プローブ
多型の検出では、一般にマイクロアレイが用いられるが、高感度な検出を行うためには、非特異的ハイブリダイゼーションを生じにくい、高性能なプローブが求められる。プローブの性能は一般的にプローブのTm値に左右されるが(Tm値が高いと非特異的ハイブリダイゼーションが起こりやすい)、Tm値はプローブの配列によって決定される。従って、一般的には、検出対象となる多型の周辺領域の配列によりプローブの性能が制約されてしまう。
しかしながら、本発明者らは、プローブの配列に、プローブ本来の性能を損なわない程度の修飾を加えることにより、プローブのTm値を調節し、プローブの性能を向上させることに成功した。
従って、本発明は、以下のプローブを提供する。
1以上の多型を有するポリヌクレオチド配列を検出するためのプローブであって、
当該配列とハイブリダイズし、且つ、少なくとも以下の要件のいずれか1つを満たすことを特徴とする、プローブ。
(1)当該配列の両端または片端に、それぞれ1つ以上の非相補的な塩基が含まれること。
(2)当該配列中に含まれる複数の多型のうち、検出目的ではない多型と対応する部分がユニバーサル塩基であること。
(3)検出目的の多型が、プローブのいずれかの末端から6塩基以下の位置にあること。
本発明において、「プローブ」とは、検体中に含まれる検出目的とする物質を捕捉することができるものをいい、デオキシリボ核酸(DNA)、リボ核酸(RNA)、ペプチド核酸(PNA)等の核酸類を示す。これらのプローブは、試験管内で酵素等により合成されたDNA又は化学合成したオリゴヌクレオチド等、合成市販品又は生細胞等から得ることができる。また、制限酵素若しくは化学的に修飾した又は切断したDNA断片も用いることができる。
プローブの長さは、一般的に10~100bp程度であるが、10~80bpが好ましく、10~50bpがより好ましく、10~35bpがさらに好ましく、12~28bpが最も好ましい。
また、検出対象である「1以上の多型を有するポリヌクレオチド配列」とは、検体に含まれるポリヌクレオチドであって、その塩基配列のなかに1以上、2以上、あるいは3以上の多型を有するものを意味する。
検出対象であるポリヌクレオチドは、おもにヒト検体に由来するものであるが、増幅反応が可能であればどのような生物種を用いてもよい。
検体は、いかなる組織由来の細胞、血液、体液であってもよい。検体の具体例としては、ヒトの脳、心臓、肺、脾臓、腎臓、肝臓、膵臓、胆嚢、食道、胃、腸、膀胱及び骨格筋等の各種組織由来の細胞、血液並びに体液が挙げられる。より詳細には、血液、髄液、尿、喀痰、胸水、腹水、胃液及び水疱内体液等が挙げられる。
検出対象であるポリヌクレオチドは、マイクロアレイに供する前に精製しておくこともできる。ポリヌクレオチドの精製方法については、例えば、Maniatisらの記載(Molecular Cloning: A Laboratory Manual,Cold Spring Harbor,NY,pp280,281,1982)に準ずる種々の技術が採用できる。
特徴(1):検出対象である多型を含むポリヌクレオチド配列の両端または片端に、それぞれ1つ以上の非相補的な塩基が含まれること
一般に、グアニン(G)とシトシン(C)の含量が多い「GC リッチ」なポリヌクレオチドは、Tm値が高く、非特異的ハイブリダイゼーションを起こしやすい。
そこで、本発明者らは、プローブとして使用するポリヌクレオチドがGC リッチ領域を含む場合、同領域の両端にGC リッチ配列と非相補的な塩基を含ませることにより、プローブと検出対象ポリヌクレオチドとの間にあえてミスマッチを生じさせ、それによってプローブのTm値を下げることができることを発見した。
「非相補的な塩基」とは、検出対象であるポリヌクレオチド配列上の対応する塩基とミスマッチを生じる塩基であれば何でもよい。例えば、検出対象であるポリヌクレオチド配列上の対応する塩基が「C」であれば、非相補的な塩基は「A」、「T」、「C」のいずれでもよい。検出対象であるポリヌクレオチド配列上の対応する塩基が「G」であれば、非相補的な塩基は「A」、「T」、「G」のいずれでもよい。また、検出対象であるポリヌクレオチド配列上の対応する塩基が「A」であれば、非相補的な塩基は「A」、「C」、「G」のいずれでもよい。さらに、検出対象であるポリヌクレオチド配列上の対応する塩基が「T」であれば、非相補的な塩基は「T」、「C」、「G」のいずれでもよい。
また、両端に含まれる非相補的な塩基の数は、5’末端と3’末端とで異なっていてもよい。
本発明において「非相補的な塩基」は、検出対象多型を含むポリヌクレオチド配列の両端部、あるいは多型を含むGC リッチ配列の両端部に含まれる。例えば、検出対象多型を含むポリヌクレオチド配列が「GGCGCGGCGCGG」である場合(中央下線部が検出対象多型)、特徴(1)を有するプローブは、「TGCGCGGCGCGA」であってもよく、「ATGCGCGGCGCGAA」であってもよく、「ATGGCGCGGCGCGGAA」であってもよい。
好ましくは、「非相補的な塩基」は、両端部のそれぞれに1塩基以上、2塩基以上、又は3塩基以上含まれる。
本発明において、GC リッチ領域とは、塩基配列全体に占めるG及びCの含量が50%以上、55%以上、60%以上、61%以上、62%以上、63%以上、64%以上、65%以上、70%以上、75%以上、80%以上、85%以上、90%以上又は95%以上である配列領域を意味する。
特徴(2):検出対象である多型を含むポリヌクレオチド配列中に含まれる複数の多型のうち、検出目的ではない多型と対応する部分がユニバーサル塩基であること
この特徴を有するプローブは、検出対象であるポリヌクレオチド配列中に、検出対象である第1の多型に加え、非検出対象である第2の多型が含まれる場合に有用である。
この場合、プローブと検出対象ポリヌクレオチドとの結合力が、第1の多型の組み合わせ以外に、第2の多型の組み合わせにより変化するため、本来の検出対象である第1の多型について検出感度が低下する。
このポリヌクレオチド配列をそのままプローブの配列として用いた場合、第1の多型部分において検出対象ポリヌクレオチドがプローブとマッチするが、第2の多型部分ではマッチしない(ミスマッチする)場合と、第1の多型部分において検出対象ポリヌクレオチドがプローブとマッチしない(ミスマッチする)が、第2の多型部分ではマッチする場合が起こり得る。後者は第1の多型がマッチしないにもかかわらず、前者と同じレベルの結合力で、プローブと検出対象ポリヌクレオチドがハイブリダイズするため、前者と同様の陽性シグナルを発することになる。
従って、上記のケースでは、前者(真の陽性)と、後者(偽陽性)とを区別することができない。
そこで、第2の多型の影響を無力化するため、本発明のプローブは、第2の多型に対応する部分にユニバーサル塩基を含むことを特徴とする。
本発明において、ユニバーサル塩基とは、天然の核酸塩基、すなわち、アデニン、グアニン、チミン、シトシン、ウラシルのいずれとも塩基対を形成しない塩基を意味する。
このようなユニバーサル塩基の例としては、5−ニトロインドール、3−ニトロピロール、7−アザインドール、6−メチル−7−アザインドール、ピロールピリジン、イミダゾピリジン、イソカルボスチリル、プロピニル−7−アザインドール、プロピニルイソカルボスチリル、及びアレニル−7−アザインドールが挙げられるが、これに限定されるものではない。
あるいは、ユニバーサル塩基の例としては、そのプロピニル誘導体を含む以下の化合物のいずれか一つ以上が挙げられる。
8−アザ−7−デアザ−2’−デオキシグアノシン、8−アザ−7−デアザ−2’−デオキシアデノシン、2’−デオキシシチジン、2’−デオキシウリジン、2’−デオキシアデノシン、2’−デオキシグアノシン、及びピロロ[2,3−d]ピリミジンヌクレオシド。
さらに、ユニバーサル塩基は、その誘導体を含む以下の化合物のいずれかからなるものであってもよい。
デオキシイノシン(例えば2’−デオキシイノシン)、7−デアザ−2’−デオキシイノシン、2’−アザ−2’−デオキシイノシン、3’−ニトロアゾール、4’−ニトロインドール,5’−ニトロインドール、6’−ニトロインドール、4−ニトロベンゾイミダゾール、ニトロインダゾール(例えば5’−ニトロインダゾール)、4−アミノベンゾイミダゾール、イミダゾ−4,5−ジカルボキサミド、3’−ニトロイミダゾール、イミダゾール−4−カルボキサミド、3−(4−ニトロアゾール−1−イル)−1,2−プロパンジオール、及び8−アザ−7−デアザアデニン(ピラゾロ[3,4−d]ピリミジン−4−アミン)。
他の例において、ユニバーサル核酸塩基は、3−メチル−7−プロピニルイソカルボスチリル基、3−メチルイソカルボスチリル基、5−メチルイソカルボスチリル基、イソカルボスチリル基、フェニル基、又はピレニル基とリボース又はデオキシリボースとを組合せることにより、ユニバーサル核酸塩基を形成してもよい。
特徴(3):検出目的の多型が、プローブのいずれかの末端から6塩基以下の位置にあること
また、本発明のプローブは、検出目的の多型が、プローブのいずれかの末端(5’末端又は3’末端)から6塩基以下の位置に存在するように設計することもできる。
このように設計されたプローブは、以下の点で有用である。
一般的に、一塩基多型検出用のプローブを設計する場合、検出目的の多型の位置を中心に5’末端、3’末端側両方に同程度の塩基長をもったプローブ設計する。しかしながら検出目的の多型の部位の5’末端または3’末端側が極端にGCリッチ領域である、またはATリッチ領域であると、検出目的の多型の位置でのプローブとのマッチ、またはミスマッチとは関係なく結合する、もしくは結合しない場合が起こりうる。
そこで検出目的の多型の位置を末端から6塩基以下の位置とし、GCリッチ領域、またはATリッチ領域を避けたプローブを用いることを特徴とする。本特徴のみではプローブの特異性を向上させることが出来ない場合においては、特徴(1)を組み合わせることもできる。
本発明のポリヌクレオチドの基となる遺伝子は、特に限定されるものではなく、例えば、G6PD遺伝子、RAB27A遺伝子、CHS1遺伝子、MTHFR遺伝子、HMGCL遺伝子、SLC2A1遺伝子、H6PD遺伝子等が挙げられる。その他個別に情報を取得するためには、疾患の情報とその原因やリスク因子である遺伝子が取得できるOMIMデータベース(http://www.ncbi.nlm.nih.gov/omim)にアクセスすればよい。
ある実施形態では、本発明のポリヌクレオチドは、ヒトβグロビン遺伝子から調製される。
本発明において、検出目的の多型を有するポリヌクレオチド配列は、グアニン及びシトシンの含有量の合計が63%以上(GC リッチ)であり、ヒトβグロビン遺伝子の第99番目~第117番目、第127番目~第142番目、第1402番目~第1416番目のヌクレオチド配列を有する。
あるいは、検出目的の多型を有するポリヌクレオチド配列は、グアニン及びシトシンの含有量の合計が45%以下(GC プア)であり、ヒトβグロビン遺伝子の第1378番目~第1399番目のヌクレオチド配列を有する。
上記領域はGC リッチ領域またはAT リッチ領域であり、この箇所における多型を検出可能なプローブを提供する。
より具体的には、本発明のプローブは、GC リッチ領域に特化したものとして、配列番号3,4,7,8,17又は18に記載の配列を有する。
一方、本発明のプローブは、GC プア領域に特化したものとして、配列番号11又は12に記載の配列を有する。
また、本発明は、配列番号3,4,7,8,11、12、17又は18に記載の配列の少なくとも1つを有する、マイクロアレイを提供する。
2.プローブ群
本発明においては、配列番号3、4、7、8、11、12、17、18と配列番号25~66に示される配列をプローブとして使用し(本発明のプローブ群)、必要に応じて、本発明のプローブ群以外の遺伝子もプローブとして使用することができる。
3.マイクロアレイ
(1)支持体
上記プローブ群を実際に使用するためには、支持体に固定化する必要である。固定化する支持体の種類は限定されず、ハイブリダイゼーション反応時に反応液にプローブが溶出(放出)することがなく、反応後にどのプローブが反応したのか特定できるものであれば、いかなるものを用いてもよい。
例えば、フィルター、ビーズ、ゲル、チップ、スライドガラス、マルチウェルプレート、メンブレンおよび光ファイバー等を挙げることができる。より詳細には、Western Blotting フィルターペーパー、ナイロンメンブレン、ポリフッ化ビニリデン製メンブレン、
ニトロセルロースメンブレン(Pierce社)、アフィニティビーズ(住友ベークライト株式会社)、MicroPlex(商標) Microspheres、xMAP Multi−Analyte LumAvidin Microspheres(Luminex社)、ダイナビーズ(株式会社ベリタス)、DNA 固定化用 96ウェルプレートキット(フナコシ社)、DNA 固定化用基板(住友ベークライト株式会社)、マイクロアレ
イ用コートスライドガラス(松波硝子工業株式会社)、ハイドロゲルスライド(パーキンエルマー社)、Sentrix(登録商標) Array Matrix(イルミナ社)等があげられる。
(2)固定化
プローブの固定化は、フィルター、メンブレン等を用いる場合は無修飾のプローブをそのままスポットし、UVランプ等の照射により固定化することができる。また、表面が化学的に活性化されているビーズ、チップ、スライドガラス、マルチウェルプレート、メンブレンおよび光ファイバー等を用いる場合は、末端が化学的に共有結合できるものを用いることが好ましい。より具体的には、5’末端又は3’末端にアミノ基等を導入したものを用いる。さらにゲル等に固定化する場合には、共重合反応可能な不飽和官能基が導入されているものを用いる。この導入基を持つことで置換(メタ)アクリルアミド誘導体やアガロース誘導体、及び架橋剤との共重合反応により、ゲルの網目構造に固定される。核酸の鎖の末端に不飽和官能基を導入する方法に関しては、例えば、国際公開第02/062817号に記載されるような公知の方法ですることができる。
本発明では、ゲル又はゲル中にプローブを固定化するのが好ましい。ゲル中に固定化することによりプローブの濃度を高くすることができるので、マイクロアレイの検出感度を高めることができるからである。また、本発明では、当該ゲルを貫通孔中に保持し、当該貫通孔を複数有する貫通孔型マイクロアレイを使用するのが好ましい。
貫通孔型マイクロアレイは、薄片プレートに貫通孔を形成して得ることもできるが、プローブを固定化したゲル担体をその種類毎に別々の中空繊維等管状体の中空部内に保持させ、そのすべての中空繊維等管状体を集束させ固定した後、繊維の長手方向で切断を繰り返すことにより得られるマイクロアレイが好ましい。安定した品質のマイクロアレイを大量生産することができるからである。このようにして、それぞれのプローブが独立した状態(1種類のプローブが1つの貫通孔内に固定化された状態)で、各貫通孔内に固定化されたマイクロアレイを得ることができる。
以下、貫通孔型マイクロアレイの製造方法の一態様について説明する。当該マイクロアレイは、下記(i)~(iv)の工程を経て製造することができる。
工程(i):複数本の中空繊維を、中空繊維の各繊維軸が同一方向となるように3次元に配列し、その配列を樹脂で固定することにより、中空繊維束を製造する工程
貫通孔を形成する方法に特に限定はなく、例えば、特開2001−133453号公報に記載されたような中空繊維を同軸方向に配列させた配列体を作製後、樹脂で固める方法を利用することができる。中空繊維は、種々の材料を用いることができるが、有機材料が好ましい。
有機材料からなる中空繊維としては、例えば、ナイロン6、ナイロン66、芳香族ポリアミド等のポリアミド系中空繊維、ポリエチレンテレフタレート、ポリブチレンテレフタレート、ポリ乳酸、ポリグリコール酸、ポリカーボネート等のポリエステル系中空繊維、ポリアクリロニトリル等のアクリル系中空繊維、ポリエチレンやポリプロピレン等のポリオレフィン系中空繊維、ポリメタクリル酸メチル等のポリメタクリレート系中空繊維、ポリビニルアルコール系中空繊維、ポリ塩化ビニリデン系中空繊維、ポリ塩化ビニル系中空繊維、ポリウレタン系中空繊維、フェノール系中空繊維、ポリフッ化ビニリデンやポリテトラフルオロエチレン等からなるフッ素系中空繊維、ポリアルキレンパラオキシベンゾエート系中空繊維等が挙げられる。中空繊維は多孔質であってもよく、溶融紡糸法又は溶液紡糸法に延伸法、ミクロ相分離法、抽出法等の公知の多孔化技術を組み合わせることにより得ることができる。多孔度は特に限定されるものではないが、繊維材料単位長さ辺りに固定化されるプローブの密度を高めるという観点から、比表面積が大きくなるように高い多孔度であることが望ましい。中空繊維の内径は任意に設定できる。好ましくは10~2000μm、より好ましくは150~1000μmとすることができる。
当該中空繊維の製造方法は限定されず、特開平11−108928号公報に記載されたような公知の方法で製造することができる。例えば、溶融紡糸法が好ましく、ノズルとしては馬蹄型やC型ノズル、2重管ノズル等を使用することができる。本発明においては、連続した均一な中空部を形成させることができる点で2重管ノズルを用いるのが好ましい。
また、必要に応じて、中空繊維にはカーボンブラック等の黒色顔料を適量含有させたものを用いることもできる。黒色顔料を含有することにより、検出する際にゴミ等の夾雑物由来の光学的ノイズを軽減することができたり、樹脂の強度を上げたりすることができる。顔料の含有量は限定されず、中空繊維のサイズやマイクロアレイの使用目的等に応じて適宜選択することができる。例えば、0.1~10質量%、好ましくは0.5~5質量%、より好ましくは1~3質量%とすることができる。
ブロック体の製造は配列体の配列が乱れないように接着剤等の樹脂で固定する方法が利用できる。例えば、粘着シート等のシート状物に複数本の中空繊維を所定の間隔をもって平行に配置し、シート状とした後、このシートを螺旋状に巻き取る方法(特開平11−108928号公報参照)が挙げられる。
また、複数の孔が所定の間隔をもって設けられた多孔板2枚を孔部が一致するように重ねあわせ、それらの孔部に、中空繊維を通過させ、2枚の多孔板の間隔を開き、2枚の多孔板間の、中空繊維の周辺に硬化性樹脂原料を充満させ硬化させる方法(特開2001−133453号公報)が挙げられる。
硬化性樹脂原料としては、ポリウレタン樹脂、エポキシ樹脂等の有機材料からなるものが好ましい。具体的には、有機高分子等から構成される1種類以上の材料から形成されているものが好ましい。有機高分子としては、ポリウレタン、シリコン樹脂、エポキシ樹脂等のゴム材料や、ナイロン6、ナイロン66、芳香族ポリアミド等のポリアミド系樹脂、ポリエチレンテレフタレート、ポリブチレンテレフタレート、ポリ乳酸、ポリグリコール酸、ポリカーボネート等のポリエステル系樹脂、ポリアクリロニトリル等のアクリル系樹脂、ポリエチレンやポリプロピレン等のポリオレフィン系樹脂、ポリメタクリル酸メチル等のポリメタクリレート系樹脂、ポリビニルアルコール系樹脂、ポリ塩化ビニリデン系樹脂、ポリ塩化ビニル系樹脂、フェノール系樹脂、ポリフッ化ビニリデンやポリテトラフルオロエチレン等からなるフッ素系樹脂、ポリアルキレンパラオキシベンゾエート系樹脂等が挙げられる。有機高分子にはカーボンブラック等の黒色顔料を適量含有させることもできる。黒色顔料を添加することにより、検出する際にゴミ等の夾雑物由来の光学的ノイズを軽減することができたり、また、樹脂の強度を上げたりすることができる。顔料の含有量は限定されず、中空繊維のサイズやマイクロアレイの使用目的等に応じて適宜選択することができる。例えば、0.1~10質量%、好ましくは0.5~5質量%、より好ましくは1~3質量%とすることができる。
本発明で配列する中空繊維の数、すなわちスポットの数は限定されず、目的とする実験等に応じて適宜選択することができる。従って、中空繊維同士の距離も、マイクロアレイの面積と配列する中空繊維の数等に応じて適宜選択することができる。
工程(ii):プローブ群を含むゲル前駆体溶液を中空繊維束の各中空繊維の中空部に導入する工程
中空糸内へ充填するゲル材の種類は、特に限定されず、天然物から得られるゲル材であれば、アガロース、アルギン酸ナトリウム等の多糖類の他、ゼラチン、ポリリジン等のタンパク質等が利用できる。合成高分子としては、例えば、ポリアクリロイルスクシンイミド等反応性官能基を有するポリマーと、反応性を示す架橋剤を反応させて得られるゲルが利用できる。他には、アクリルアミド、N、N−ジメチルアクリルアミド、N−イソプロピルアクリルアミド、N−アクリロイルアミノエトキシエタノール、N−アクリロイルアミノプロパノール、N−メチロールアクリルアミド、N−ビニルピロリドン、ヒドロキシエチルメタクリレート、(メタ)アクリル酸及びアリルデキストリン等の重合性モノマーを単量体として、多官能性単量体、例えば、メチレンビス(メタ)アクリルアミド、ポリエチレングリコールジ(メタ)アクリレート等との共重合により得られる合成高分子ゲルが好ましい。
本発明のマイクロアレイに用いるゲルの濃度は特には限定されず、使用するプローブの長さや量に応じて適宜選択することができる。例えば、単量体成分の濃度に換算して、2~10質量%が好ましく、より好ましくは3~7質量%、更により好ましくは3.5~5質量%である。2質量%以上とするのは、プローブが確実に固定化することができ、標的物質の検出を効率良く行うことができるからである。また、10質量%以下とするのは、それ以上濃度を高くしても飛躍的な効果が得られにくいからである。
合成高分子ゲルを前記の貫通孔基板のマイクロアレイに保持させる場合は、前記ブロックに合成高分子のゲル前駆体溶液を充填させた後、ブロック内でゲル化させて保持させることができる。ゲル前駆体溶液をブロックの貫通孔内に充填する方法は、例えば、微細な針を有するシリンジに前記溶液を吸引し、各中空繊維の中空部に針を差し込むことにより導入することができる。また、中空繊維束の固定されている端部の中空部を封止し、もう一方の固定されていない端部の中空部を開放しておく。次にメタクリル基等の重合反応点を末端に持つ核酸プローブを含むゲル前駆体溶液を調製し、該ゲル前駆体溶液及び前記中空繊維束をデシゲーター内に設置し、次いで中空繊維束の中空繊維が固定されていない端部を、この溶液中に浸し、デシゲーター内を減圧状態にした後、常圧に戻すことにより、中空繊維の溶液に浸した端部より、この溶液を中空繊維中空部へ導入することができる。
工程(iii):中空繊維束の中空部に導入したゲル前駆体溶液を反応させ、プローブを含むゲル状物を中空繊維の中空部に保持する工程
中空繊維の中空部に導入されたゲル前駆体溶液を重合させることにより、プローブを含むゲル状物を中空繊維の中空部に保持させる。重合条件は特には限定されず、使用したゲル前駆体の種類等により適宜選択することができる。例えば、アクリルアミド系の単量体であれば、ラジカル開始剤を使用して重合することができ、好ましくは、アゾ系開始剤を利用した熱重合反応により重合させることができる。
プローブの種類やサイズは限定されず、検出対象となる物質又は化合物の種類に応じて適宜選択することができる。
工程(iv):中空繊維束を繊維の長手方向に交叉する方向で切断して薄片化する工程
切断方法は、薄片化することができれば限定されない。例えば、ミクロトーム、レーザー等により行うことができる。得られる薄片の厚みは限定されず、実験の目的等に応じて適宜選択することができる。例えば、5mm以下、好ましくは0.1~1mmとすることができる。
(3)βグロビン遺伝子の変異の検出
本発明において、βグロビン遺伝子の変異を検出するとは、βグロビン遺伝子配列中の変異部分を有する塩基部位、配列を特定することを意味し、また、複数の特定された対立遺伝子からどの対立遺伝子の組(二倍体の生物)であるかを判定することを意味する。
(a)まず、ヒトゲノムDNAを含む検体と、核酸増幅用プライマーセット、ヌクレオチド単体及びDNA伸長酵素を含む反応溶液とを接触させればよい。
<検体(核酸増幅の鋳型となる核酸)>
検体(核酸増幅の鋳型となる核酸)とは、本発明において検出する目的となる遺伝子配列すなわちβグロビン遺伝子配列を含む核酸をいい、βグロビン遺伝子配列の断片が含まれ、以下に述べる増幅反応が進行するものであればどのような形態の核酸でもよい。
検体の由来は、ヒト由来であり増幅反応が可能であればどのようなものを用いてもよい。 検体はまた、いかなる組織由来の細胞、血液、体液を使用してもよい。例えば、脳、心臓、肺、脾臓、腎臓、肝臓、膵臓、胆嚢、食道、胃、腸、膀胱、骨格筋等の各種組織由来の細胞、血液、体液が挙げられる。より詳細には、例えば、血液、髄液、尿、喀痰、胸水、腹水、胃液、水疱内体液等が挙げられる。
また、検体は、後述する核酸増幅を行う前に、当該増幅に用い得るDNA含有試料として
調製及び精製しておくことが好ましい。当該調製及び精製は、公知の核酸抽出法に従って行うことができ、例えば、Maniatisらの記載(Molecular Cloning: A Laboratory Manual,Cold Spring Harbor,NY,pp280,281,1982)に準ずる種々の技術を用いることができ
る。
<核酸増幅用プライマーセット、プローブ位置>
本発明はβグロビン遺伝子の変異を検出するためのプローブセットに関し、NCBI Reference Sequence:NC_000011.9(配列長135006516塩基)の相補鎖配列上にコードされているβグロビン遺伝子配列の変異を検出する。
通常、検出しようとする核酸の変異箇所はあらかじめ決めておくことが検出の点から好ましい。プライマー対は、検出しようとする変異箇所を含んだ増幅産物が生成されるのであれば、どこに設計してもよい。例えばエキソン1、2に含まれる変異箇所をまとめて複数検出する場合には、エキソン1より上流のフォワードプライマーとエキソン2下流のリバースプライマーで核酸増幅を行い、その増幅産物を検出すればよい。また複数の領域を一度に検出する場合には複数のプライマー対を用いることができる。この場合、増幅する段階で非特異的な核酸断片が生成していないかどうか条件設定をする段階で確認しておくことが好ましい。一度条件を決めてしまえば、その条件で再現性よく検出することができる。
プローブとなるオリゴヌクレオチドの塩基配列は、増幅産物配列(プライマーセットで挟まれる領域)の内部に含まれるようにプローブ配列を決定する。プローブは通常、15~35ヌクレオチド程度の長さで設定し、検出する変異領域1つに対して通常1組(野生型検出用プローブと変異型検出用プローブの2種)又はそれ以上(1組以上)のプローブを必要とする。
後の検出が容易になるように、使用するプライマーセットはあらかじめその末端を蛍光物質(Cy3、Cy5等)やビオチン等であらかじめ標識しておくとよい。標識方法は特に限定されず、増幅反応において著しく反応が阻害される等の現象がみられなければどのような方法でもよい。反応後、酵素との複合体、例えばストレプトアビジンアルカリフォスファターゼコンジュゲートをさらに反応させ、基質を加えることにより発色させることも可能である。
<増幅反応>
上記核酸増幅の鋳型となる核酸(検体)を鋳型にして、核酸増幅反応により、βグロビン遺伝子の変異箇所で検出しようとする領域の核酸断片を増幅させる。核酸の増幅方法としてはPCR法、LAMP法、ICAN法、TRC法、NASBA法、PALSAR法等様々な方法を使用することができる。核酸の検出上特に問題が生じなければいずれの方法も核酸増幅反応に用いることができるが、これらの中でも簡便さの観点からPCR法が好ましい。
核酸増幅反応に用いる温度制御装置は、市販のサーマルサイクラーを用いることができる。例えば、GeneAmp 9600やGeneAmp 9700(ライフテクノロジーズジャパン株式会社)、T Professionalシリーズ(バイオメトラ社)等を用いることができるが、熱伝導性、蓋の形状について問題が生じなければどのような型式のものであってもよい。
<増幅反応で用いるヌクレオチド単体>
ヌクレオチド単体は、通常の増幅反応で用いるデオキシリボヌクレオチド三リン酸等が挙げられる。これもプライマーセットと同様、後の検出が容易になるような誘導体を用いることも可能であるが、増幅反応を阻害しないものを使用することが好ましい。
<増幅反応で用いるDNA伸長酵素、その他>
DNA伸長酵素は、通常のPCR法に用いられるものと同様に、耐熱性細菌に由来するDNAポリメラーゼであるTaqDNAポリメラーゼ、TthDNAポリメラーゼ、PfuDNAポリメラーゼ等を使用することができる。
使用可能な酵素やキットとしては、Hot StarTaq DNA Polymerase(QIAGEN社製)、PrimeStarMax DNAポリメラーゼ(タカラバイオ社)、SpeedSTAR HS DNAポリメラーゼ(タカラバイオ社)、KOD−Plus−Neo(東洋紡社)、KAPA2G FastHotStartPCR キット(日本ジェネティックス(株)社)、AmpDirect キット(島津製作所)等が挙げられ、その他には直接血
液(体液等)から核酸増幅反応ができるものであれば操作が簡便になるのでより好ましい。
上記の構成要素を混合する方法としては、酵素が失活しない、液が泡立ってチューブから漏えいしないように混合すればどのような混合の仕方でもよい。通常は上記すべての構成成分を0.2mL程度の大きさのPCR用チューブに分注しボルテックスミキサーで混合した後、蓋についた溶液を落とすために軽く遠心(スピンダウン)すればよい。またホットスタートPCRを行う場合においては、混合時に酵素が活性化されない条件で混合を行う。
次に、(b)上記(a)で得られた反応液を核酸増幅反応に供すればよい。
核酸増幅反応は例えばPCR反応で増幅する場合においては、90℃~98℃で5分間程度テンプレートとなる核酸を解離させる酵素を活性化させた後、94℃30秒(核酸の解離)、60℃30秒(プライマーのアニーリング)、72℃30秒(プライマーからの伸長反応)程度のサイクルを25~50サイクル繰り返すことにより指数関数的に核酸を増幅させることができる。またPCR反応でない等温条件での核酸増幅反応を行う場合においては、40℃~65℃程度の一定温度でインキュベートすることにより増幅した核酸を得ることができる。
(c)続いて、(b)で得られた核酸断片を、本発明のマイクロアレイに接触させることにより、検体中の目的とする核酸を検出することができる。
工程(c)においては、核酸増幅反応液を精製することなく、直接ハイブリダイゼーション溶液を加えて、マイクロアレイに接触させることができる。ハイブリダイゼーション溶液とは増幅核酸が、マイクロアレイに固定化されたプローブとハイブリダイゼーション反応を可能にさせる溶液である。
より詳細には、Tris/HCl buffer等のバッファー溶液にNaCl溶液、MgCl2溶液等の塩を混合した溶液やSSC溶液、SDSやTween20等の界面活性剤を混合したものである。本発明で使用するプローブとの反応を行う場合においては、SDS等、冷却時に界面活性剤の結晶が析出しないTNT buffer(Tris/HCl buffer溶液、NaCl溶液、Tween溶液の混合溶液)を用いることが好ましい。
Tris/HCl又はNaClの濃度は、終濃度としてそれぞれ0.06M~0.48Mが好ましく、0.12M~0.24Mがより好ましい。Tweenは終濃度として、0.01~0.2質量%、好ましくは0.02~0.15質量%、より好ましくは0.03~0.12質量%とすることができる。
また、接触時の温度は45~65℃が好ましく、50~55℃がより好ましく、さらに45~70℃が好ましく、またさらに50~65℃が好ましい。接触させる時間はハイブリダイゼーション反応が起こり、変異が検出できれば限定さないが、非特異的な反応を抑えるためには短いほど良い。例えば、接触時間は15分~4時間、好ましくは20分~3時間、より好ましくは30分~2時間とすることができる。
<核酸(増幅産物)の検出>
上記工程(c)によりマイクロアレイ中のプローブで捕捉された核酸を検出する。
検出方法としては捕捉された核酸が検出されれば限定されず、公知の方法を使用することができる。例えば、蛍光物質や発光物質を標識基質として使用し、発色測定や蛍光強度測定を行う方法、目視による方法等を用いることができる。
より詳細には、フルオロイメージングアナライザーやCCDカメラ等を用いて捕捉された核酸の有無及び定量を行うことができる。近年多用されつつあるPCR反応随時定量装置等を用いて蛍光量を経時的にモニタリングすることにより、より信頼性の高い核酸の定量ができる。
さらに、酵素反応を利用する又は利用しない発色試薬等を用いて発色を行うこともできる。このような方法では、目視で直接観察したり光学スキャナーでスキャンしたりすることが可能である。
本発明の核酸の検出方法は、配列表で開示したβグロビン遺伝子の変異30箇所の解析への適用が挙げられるが、さらには適切なプローブを設計・使用することによって本発明で開示した変異箇所以外の箇所についての検出キットを作製することも可能である。
(4)キット
本発明において、プライマーセット及び本発明のプローブ群を有するマイクロアレイを、βグロビン遺伝子の変異を検出するためのキットとして使用することも可能である。プライマーセットとしては、配列番号21で示されるオリゴヌクレオチドプライマーと配列番号22で示されるオリゴヌクレオチドプライマーのセット、又は配列番号23で示されるオリゴヌクレオチドプライマーと配列番号24で示されるオリゴヌクレオチドプライマーのセットをより好適に使用することができる。
4.マイクロアレイ・プローブの評価方法
既に述べたように、マイクロアレイで多型の検出を行う場合、使用するプローブが非特異的ハイブリダイゼーションを起こさないことが好ましい。つまり、非特異的ハイブリダイゼーションを起さないプローブは、性能が高いものと評価される。
そこで、本発明は、プローブの性能を定量的に評価する方法として、以下の方法を提供する。
以下の工程を含む、マイクロアレイ・プローブの評価方法。
(1) 第1の多型検出用プローブがハイブリダイズして得られるシグナル強度を表すY軸と、第2の多型検出用プローブがハイブリダイズして得られるシグナル強度を表すX軸とを含む蛍光座標系において、第1の多型用コントロール核酸を、第1及び第2の多型検出用プローブからなる多型検出用プローブペアとハイブリダイズして得られた蛍光座標をプロットする工程、
(2) 前記Y軸とX軸との交点Oと、前記工程(1)でプロットされた蛍光座標とを通る直線の傾きに反比例する値を補正値Cと定める工程、
(3) 工程(1)及び(2)を複数の多型検出用プローブペアについて行い、各プローブ間で補正値Cを比較し、補正値Cが最小となるプローブペアを第1の多型検出に適したプローブとして決定する工程。
本発明において、第1の多型と第2の多型は、同一の多型における異なる対立遺伝子である。すなわち、第1の多型は、第1の対立遺伝子であり、第2の多型は、前記第1の対立遺伝子に対応する第2の対立遺伝子である。
以下、各工程の概要を説明する。
工程(1):プロット工程
まず、工程(1)において、第1の多型用コントロール核酸が、第1及び第2の多型検出用プローブからなる多型検出用プローブペアとハイブリダイズして得られるシグナル強度を蛍光座標系にプロットする。本発明の蛍光座標系において、Y軸は第1の多型検出用プローブがハイブリダイズして得られるシグナル強度を表し、X軸は第2の多型検出用プローブがハイブリダイズして得られるシグナル強度を表す。ここでY軸とX軸の交点をOとする。また、Y軸とX軸とは直交していていもよく、直交していなくてもよい。
前記プロットにより第1の多型検出用プローブの蛍光特性を表す蛍光座標P(x1、y1)が得られる。
非特異的なハイブリダイゼーションを起こさない理想的なプローブの蛍光座標Pはx1=0、y1>0となる(図1:パネルA)。
しかしながら、実際には多くのプローブが、ある程度の非特異的ハイブリダイゼーションを生じる。従って、多くのプローブでは、蛍光座標Pはx1>0かつy1>0となる(図1:パネルB)。
ハイブリダイゼーションはハイブリダイゼーション溶液中で行われる。ハイブリダイゼーション溶液とはコントロール核酸とプローブとのハイブリダイゼーション反応を可能にさせる溶液であるが、より具体的には、Tris/HCl buffer等のバッファー溶液にNaCl溶液、MgCl2溶液等の塩を混合した溶液やSSC溶液、SDSやTween20等の界面活性剤を混合したものがある。一般的に反応を行う場合においては、SDS等、冷却時に界面活性剤の結晶が析出しないTNT buffer(Tris/HCl buffer溶液、NaCl溶液、Tween溶液の混合溶液)を用いることが好ましい。またその終濃度は0.06M~0.48Mが好ましく、より好ましくは終濃度が0.12M~0.24Mである。また接触時の温度は、45℃~70℃が好ましく、より好ましくは50℃~65℃である。接触時間はハイブリダイゼーション反応が起こり検出できる範囲であれば短いほど好ましい。通常15分~4時間、好ましくは20分~3時間、より好ましくは30分~2時間である。
シグナルとは、前述のハイブリダイゼーションの結果、プローブで捕捉されたコントロール核酸の量を数値化したものである。一般的には、プローブとハイブリダイズさせる核酸試料に蛍光物質や発光物質を結合させ、プローブ領域から発せられる蛍光や発色の強度を測定することによりシグナルを得ることができる。具体的には、シグナルは、フルオロイメージングアナライザーやCCDカメラ等を用いて得ることができる。
プローブに「対応した」シグナルとはシグナル内にバックグラウンド由来のシグナルを含みうるが、プローブに「由来した」シグナルとはプローブ本来の特異性に由来するシグナルを意味する
工程(2):補正値の決定
次に、プロットされた蛍光座標Pと交点Oとを通る直線Lを求め、この直線Lの傾きに反比例する値を補正値C(C>0)としてもよい。
具体例として、補正値Cは、直線LとX軸とがなすラジアン角度α(0≦α≦π/2)に反比例するものであってもよい(図1:パネルC)。つまり、蛍光座標PをY軸上に存在するように補正する場合、角度αを(π/2)÷α倍増幅させる必要があるが(図1:パネルD)、この増幅度に基づき、補正値C=(π/2)÷α(C≧1)と定めることもできる。
工程(3):プローブペアの比較
通常、1つの多型を検出するためには、複数の候補のプローブが用意される。従って、複数の候補プローブについて上記工程(1)及び(2)を行い、各プローブの補正値Cを定める必要がある。
このようにして得られた補正値Cを比較することにより、候補プローブの性能を比較評価することができる(図1:パネルE)。
すでに述べた通り、理想的なプローブでは、蛍光座標PはY軸上に存在するため、α=π/2となる。従って、理想的なプローブでは補正値C=(π/2)÷(π/2)=1となる。
一方、ある程度の非特異的ハイブリダイゼーションを生じるプローブの場合、α<π/2となるので、補正値C>1となる。例えば、α=π/4の場合、補正値C=2となり、α=π/6の場合、補正値C=3となる。
従って、本発明の方法では、補正値Cの値が小さいほど、そのプローブは高性能である判断される。すなわち、補正値Cが最小となるプローブ(つまり角度αが最大)が第1の多型検出に適したプローブとして決定される。例えば、図1パネルEの例ではプローブペアNo.3が第1の多型検出に適したプローブとして決定される。
以上に述べた工程には種々の改変を加えてもよい。
例えば、工程(1)において、コントロール核酸とプローブとのハイブリダイズを2回以上繰り返し、2点以上の蛍光座標を獲得してもよい(図2:パネルA:この場合は3点の蛍光座標)。この場合、獲得した2点以上の蛍光座標の代表値Mを求め、工程(2)における直線Lは、交点Oと代表値Mとを通る中央直線であってもよい(図2:パネルB)。ここで代表値とは複数の値を代表する値である。例えば、平均値、中央値又は重み付けした平均値などが挙げられるが、外れ値に対する頑強性の点で中央値が好ましい。
さらに、工程(1)において、交点Oと蛍光座標とを通る各直線のうち(蛍光座標が2点以上存在するので、直線も2本以上存在する)、前記中央直線との傾きの差がある直線を選択し、これを誤差直線(傾きの差が最大の直線を選択する場合は第1の誤差直線とする)と定めてもよい(図2:パネルB)。
第1の誤差直線を定める場合、工程(2)は、
(a)前記中央直線とX軸との間の角度α(ラジアン)を求め、
補正値C=π/2÷αを求める処理(図2:パネルC)、
(b)前記中央直線と誤差直線(傾きの差が最大の直線を選択する場合は第1の誤差直線とする)とがなす角度を誤差角θ(ラジアン)と定め、
さらに、補正誤差角θ’(ラジアン)=θ(ラジアン)×補正値Cと定める処理
を含むものとする。
誤差角は必要に応じて上記の定数倍をしてもよい。また、差がある直線として、差が最も大きな直線を第1の誤差直線と定めてもよく、複数の差がある直線との角度差から信頼区間を加味した誤差角の範囲を定めてもよい。
他方、第2の多型用コントロール核酸を用いて、第2の多型検出用プローブに対し、上記工程(1)~(3)に相当する工程(4)~(6)を行ってもよい。
具体的には、工程(4)~(6)は以下のとおりである。
(4)第2の多型用コントロール核酸を、第1及び第2の多型検出用プローブからなる多型検出用プローブペアとハイブリダイズして得られた蛍光座標をプロットする工程、
(5) 交点Oと、工程(4)でプロットされた蛍光座標とを通る直線の傾きに比例する値を補正値C2と定める工程、
(6) 工程(4)及び(5)を複数の多型検出用プローブペアについて行い、各プローブ間で補正値C2を比較し、補正値C2が最小となるプローブペアを第2の多型検出に適したプローブとして決定する工程。
工程(4):プロット工程
工程(4)において、第2の多型用コントロール核酸が、第1及び第2の多型検出用プローブからなる多型検出用プローブペアとハイブリダイズして得られるシグナル強度を蛍光座標系にプロットする。
前記プロットにより第2の多型検出用プローブの蛍光特性を表す蛍光座標P2(x2、y2)が得られる(図3:パネルA)。
工程(5):補正値の決定
次に、プロットされた蛍光座標P2と交点Oとを通る直線L2を求め、この直線L2の傾きに比例する値を補正値C2(C2>0)としてもよい。
具体例として、補正値C2は、直線L2とY軸とがなすラジアン角度β(0≦β≦π/2)に反比例するもの(つまり、L2の傾き(π/2−β)に比例する)であってもよい(図3:パネルB)。蛍光座標P2をX軸上に存在するように補正する場合、角度βを(π/2)÷β倍増幅させる必要があるが(図3:パネルC)、この増幅度に基づき、補正値C2=(π/2)÷β(C2≧1)と定めることもできる。
工程(6):プローブペアの比較
上記工程(3)と同様に、複数の候補プローブペアについて上記工程(4)及び(5)を行い、各プローブの補正値C2を定める必要がある。
このようにして得られた補正値C2を比較することにより、候補プローブの性能を比較評価することができる(図3:パネルD)。
すでに述べた通り、理想的なプローブペアでは、蛍光座標P2はX軸上に存在するため、β=π/2となる。従って、理想的なプローブでは補正値C2=(π/2)÷(π/2)=1となる。
一方、ある程度の非特異的ハイブリダイゼーションを生じるプローブの場合、β<π/2となるので、補正値C2>1となる。例えば、β=π/4の場合、補正値C2=2となり、β=π/6の場合、補正値C2=3となる。
従って、補正値C2の値が小さいほど、そのプローブは高性能である判断される。すなわち、補正値C2が最小となるプローブが第2の多型検出に適したプローブとして決定される。例えば、図3パネルDの例ではプローブペアNo.4’が第2の多型検出に適したプローブとして決定される。
以上に述べた工程には種々の改変をくわえてもよい。
例えば、工程(4)において、コントロール核酸とプローブとのハイブリダイズを2回以上繰り返し、2点以上の蛍光座標を獲得してもよい(図4:パネルA:この場合3点の蛍光座標)。この場合、獲得した2点以上の蛍光座標の代表値M2を求め、工程(2)における直線L2は、交点Oと代表値M2とを通る第2の中央直線であってもよい(図4:パネルB)。
ここで代表値とは複数の値を代表する値である。例えば、平均値、中央値又は重み付けした平均値などが挙げられるが、外れ値に対する頑強性の点で中央値が好ましい。
さらに、工程(4)において、交点Oと蛍光座標とを通る各直線のうち(蛍光座標が2点以上存在するので、直線も2本以上存在する)、前記第2の中央直線との傾きの差がある直線を選択し、これを誤差直線(傾きの差が最大の直線を選択する場合は第2の誤差直線とする)と定めてもよい(図4:パネルB)。
第2の誤差直線を定める場合、工程(2)は、
(a)前記第2の中央直線とY軸との間の角度β(ラジアン)を求め、
補正値C2=π/2÷βを求める処理、
(b)前記第2の中央直線と誤差直線(傾きの差が最大の直線を選択する場合は第2の誤差直線とする)とがなす角度を誤差角θ2(ラジアン)と定め、
さらに、補正誤差角θ2’(ラジアン)=θ2(ラジアン)×補正値C2と定める処理
を含むものとする。
誤差角は必要に応じて上記の定数倍をしてもよい。差がある直線として、差が最も大きな直線を第2の誤差直線と定めてもよく、また複数の差がある直線との角度差から信頼区間を加味した誤差角の範囲を定めてもよい。
また、本発明は、上記方法により評価されたプローブの補正値C(又はC2)を表示する方法を提供しプローブの性能が評価される。さらには、補正値C(又はC2)を使用して補正された座標と補正された誤差範囲を表示する方法も提供する。
本発明の評価方法では、各プローブ間の性能を容易に比較することができ、また誤差範囲を考慮して遺伝子型を判定することも可能である。
以下、実施例により本発明を更に具体的に説明するが、これらの実施例は、本発明の例示を目的とするものであり、本発明を限定するものではない。
[実施例1]
DNAマイクロアレイを用いてβグロビン遺伝子の25箇所の変異を一括して検出することを検討した。検出対象する変異の箇所を以下の表1に示した。
1.貫通穴型DNAマイクロアレイの作製
DNAマイクロアレイを以下のようにして製造した。
<1−1.プローブの調製>
プローブとなる配列番号1~18記載のオリゴヌクレオチドを合成した。
オリゴヌクレオチドの5’末端にアミノヘキシル基が導入されたオリゴヌクレオチドとして合成した。合成後、そのオリゴヌクレオチドに、無水メタクリル酸を反応させ、さらにHPLCで精製、分取することにより、表2の配列番号1~18で示される塩基配列を有する5’末端ビニル化オリゴヌクレオチドを取得した。配列の特徴として、配列番号1,2は変異c.52A>Tに近接した変異c.59A>Tの変異の影響をうけるプローブであるが、配列番号3,4は変異c.52A>Tに近接した変異c.59A>Tの変異にハイブリダイズするユニバーサル塩基としてイノシンを導入している。
同様に配列番号5,6は変異c.84_85insCに近接した変異c.79G>Aの変異の影響を受けるプローブであるが、配列番号7,8は変異c.84_85insCに近接した変異c.79G>Aの変異にハイブリダイズするユニバーサル塩基としてイノシンを導入している。
また、配列番号11,12は変異を検出するための異なる塩基の箇所がプローブの3末端から6塩基の位置にあり、配列番号17、18は両末端に「AA」を導入している。
<1−2.DNAマイクロアレイ>
本実施例では、表1に記載のプローブ(配列番号1~18)及びプローブを搭載しない箇所については核酸プローブの代わりに水を使用した核酸マイクロアレイ((ジェノパール:登録商標)、三菱レイヨン株式会社)を用いた。
2.βグロビン遺伝子の変異検出用プローブの評価
<2−1.プラスミドテンプレートDNAの作製>
NCBI Reference Sequence: NC_000011.9(配列長135006516塩基)の5246730塩基目から5248465塩基目の相補鎖配列上にβグロビン遺伝子配列がコードされている。その配列を配列番号19に示した。また、配列番号20で示すNM_000518.4| Homo sapiens hemoglobin,beta (HBB),mRNAの配列と比較することで、ゲノムDNA配列中のエキソン領域を特定した。(タンパク質コード領域51塩基目~494塩基目、exon1:1塩基目~142塩基目、エキソン2:143塩基目~365塩基目、エキソン3:366塩基目~626塩基目)
配列番号19中、斜体で示した配列箇所は配列番号21~24のプライマー配列の位置、下線で示した配列はエキソン領域、四角で囲んだ領域はUTR領域である。
βグロビン遺伝子の野生型テンプレートとして、配列番号19に示した配列を含むプラスミドを合成して用意し(株式会社BEX社の人工遺伝子合成サービスを用いてpUC57ベクターに挿入したものである)、10ng/μlに濃度を調製した。
またこれと同様に先の表1に示したHGVS nomenclatureに従った変異表記の位置に変異が入ったプラスミドDNA(25種類)を個々に用意し、それらも10ng/μlに濃度を調製した。
プライマー対<配列番号21、22、23、24>
<配列番号19>
<配列番号20>
<PCR反応>
野生型のプラスミドDNAと表1記載の番号10、13、21、23(変異c.52A>T 、c.84_85insC 、c.364G>C、c.380T>Gを含む)の変異型プラスミドDNA4種類、計5種類を鋳型とし、
配列番号21~24の2組のプライマー対を用いてPCR反応を行った。PCR反応にはKOD FX Neoキット(東洋紡社)を用いた。
<PCR反応液組成>
PCR反応にはGeneAmp9700サーマルサイクラーを用い、Maxモードで反応した。温度条件を以下に示した。
<PCR反応温度条件>
95℃ 10分間
(94℃30秒、68℃30秒、72℃30秒)×35サイクル
4℃ 反応終了
反応後の反応液100μlに以下のバッファー溶液を加え200μlとした。
その後、この溶液200μlを専用チャンバーに入れ(http://www.mrc.co.jp/genome/about/usage.htmlに記載)、引き続いてDNAマイクロアレイを入れてふたを閉め、55℃で2時間インキュベートした。
インキュベート後、チップをそれぞれ0.24M TNT buffer 10mlに55℃、20分間浸漬した。その後、引き続いて、0.24M TN buffer 10mlに55℃、10分間浸漬して洗浄を実施した。洗浄後、検出を実施した。
検出は、冷却CCDカメラ方式のDNAマイクロアレイ自動検出装置を用いた。DNAマイクロアレイをウェル上部から露光時間4秒間で撮像し、各スポットにおけるcy5の蛍光シグナルを検出した。マイクロアレイ上のプローブが搭載されていないスポットをブランクスポットとし、その蛍光強度の中央値をバックグラウンド値とした。すべてのスポットの蛍光強度からバックグランド値を減算した値を各プローブのシグナルとした。
野生型の配列を第1の多型、変異型の配列を第2の多型、第1の多型用コントロール核酸を野生型プラスミドとして、複数回実験を行った結果を表3に示した。また、表3の結果を、第1の多型検出用プローブがハイブリダイズして得られるシグナル強度を表すY軸と、第2の多型検出用プローブがハイブリダイズして得られるシグナル強度を表すX軸とを含み、X−Y軸が直交している蛍光座標系にプロットした結果を図5に示した(図5:第1・第2の多型検出用プローブのシグナル強度を表す蛍光座標系において、第1のコントロール核酸を複数回ハイブリダイズ結果をプロットし、さらにそれらの代表直線を示した図)。
図5の点線は、各々のプローブペア候補の複数(2回または3回)の実験結果の平均シグナル強度と、原点とを結ぶ直線(代表直線とする)であり、グラフ中の数式はこれらの直線の式を示している。
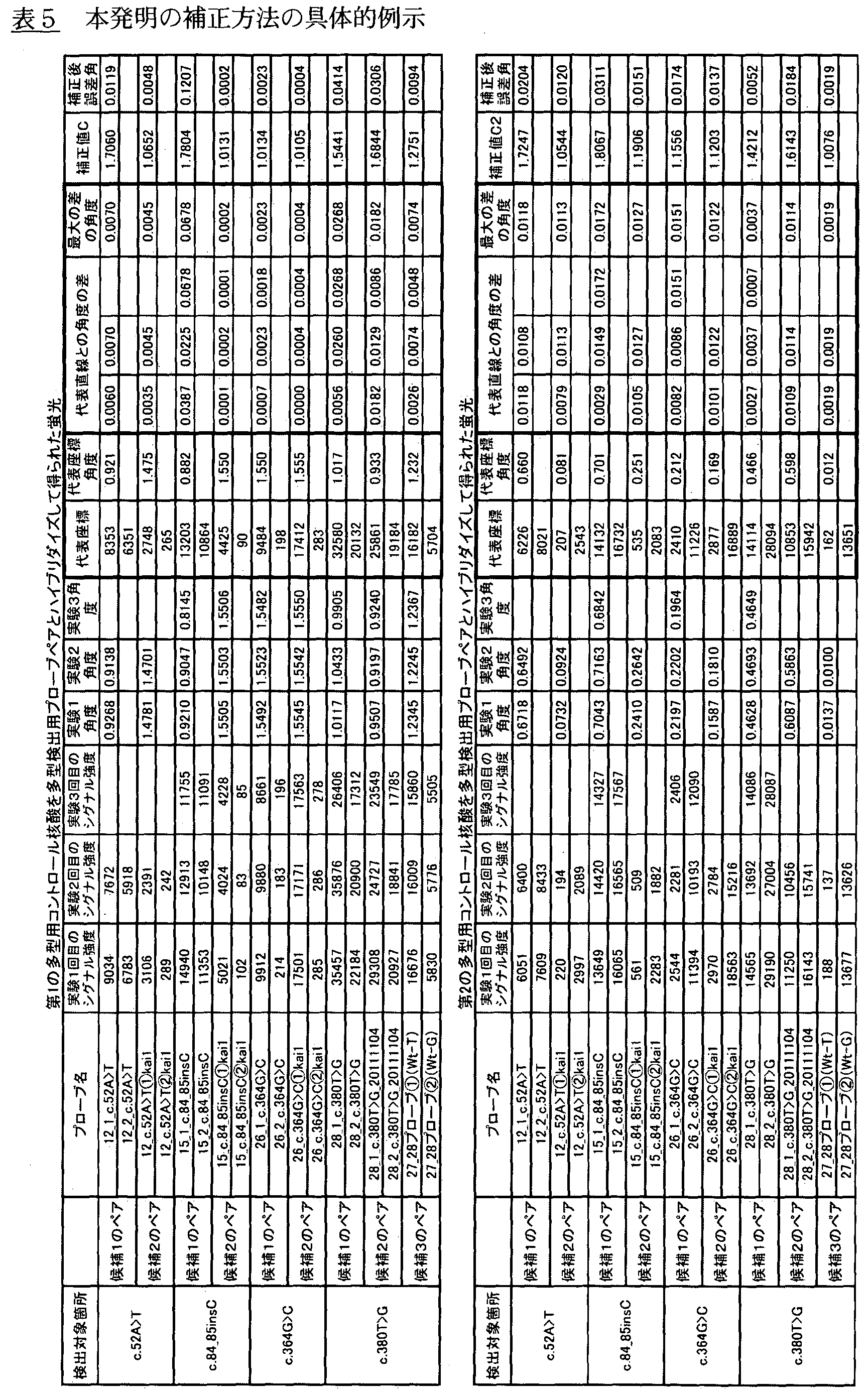
プローブの選択については、代表直線の傾きに反比例する値を補正値Cと定め、複数の多型検出用プローブペアについて行い比較し、補正値Cが最小となるものを選択する。本検討では、補正値Cはπ/2÷代表直線とX軸とのなす角度(ラジアン)で算出した。各プローブペアのうち、性能のよいプローブペアとして、
c.52A>Tの変異を検出するプローブとして、配列番号1,2のペアと配列番号3,4のペアでは、配列番号3、4のペア、
c.84_85insCの変異を検出するプローブとして、配列番号5,6のペアと配列番号7,8のペアでは、配列番号7、8のペア、
c.364G>Cの変異を検出するプローブとして、配列番号9,10のペアと配列番号11,12のペアでは、配列番号11、12のペア、
c.380T>Gの変異を検出するプローブとして、配列番号13,14のペア、配列番号15,16のペア、配列番号17,18のペアでは、配列番号17、18のペア、
をプローブ候補の中から選択することができた。
同様に、野生型の配列を第1の多型、変異型の配列を第2の多型、第2の多型用コントロール核酸を変異型プラスミドとして、複数回実験を行った結果を表4に示した。また、表3と表4の結果を、第1の多型検出用プローブがハイブリダイズして得られるシグナル強度を表すY軸と、第2の多型検出用プローブがハイブリダイズして得られるシグナル強度を表すX軸とを含み、X−Y軸が直交している蛍光座標系にプロットした結果を図6に示した(図6 図5に加え、第2のコントロール核酸を複数回ハイブリダイズ結果をプロットし、さらにそれらの代表直線を示した図)。
図6グラフ中の「第2の多型用コントロール核酸をハイブリダイズ」を含む系列は、変異型のプラスミドをハイブリダイズした結果である。点線または実線は、各々のプローブペア候補の複数(2回または3回)の実験結果の平均シグナル強度と、原点とを結ぶ代表直線である。
これらのプローブの選択については、代表直線の傾きに比例する値を補正値C2と定め、複数の多型検出用プローブペアについて行い比較し、補正値C2が最小となる第2(変異型)の多型検出に適したプローブペアを選択する。
本検討では、補正値C2はπ/2÷(π/2−代表直線とX軸とのなす角度(ラジアン))として算出した。各プローブペアのうち、性能のよいプローブペアとして、
c.52A>Tの変異を検出するプローブとして、配列番号1,2のペアと配列番号3,4のペアでは、配列番号3、4のペア、
c.84_85insCの変異を検出するプローブとして、配列番号5,6のペアと配列番号7,8のペアでは、配列番号7、8のペア、
c.364G>Cの変異を検出するプローブとして、配列番号9,10のペアと配列番号11,12のペアでは、配列番号11、12のペア、
c.380T>Gの変異を検出するプローブとして、配列番号13,14のペア、配列番号15,16のペア、配列番号17,18のペアでは、配列番号17、18のペア、
をプローブ候補の中から選択することができた。
以上、これまで示した補正値C、C2のグラフを図7に示した。
プローブの評価に引き続き、遺伝子型判定の際に有用となる誤差範囲について以下の表5のように設定した。第1のコントロール核酸または第2のコントロール核酸を2回以上の繰り返して得られたシグナル強度から平均値を算出し、そのプローブペアが与える代表座標とした。また代表座標と原点を通る直線を代表直線としX軸と代表直線との角度を代表座標角度として個々のデータと原点と結ぶ直線と代表直線との角度を算出し(ラジアン単位)、最大の角度を誤差角度とした。また、補正値C、C2、誤差角度を用いて補正した前後のプローブ性能データについて図8に示した。
DNAマイクロアレイを用いてβグロビン遺伝子の25箇所の変異を一括して検出ため、配列番号3、4、7、8、11、12、17、18と配列番号25~66に示されるプローブを搭載したアレイを作製した。
検出対象とする変異の箇所は実施例1の表1と同様であり、DNAマイクロアレイも実施例1と同様に作製した。
<PCR反応>
表1記載の番号1~25の変異型プラスミドDNAを鋳型とし、配列番号21~24の2組のプライマー対を用いてPCR反応を行った。PCR反応にはアンプダイレクトプラスキット(島津製作所)を用いた。
<PCR反応液組成>
PCR反応にはGeneAmp9700サーマルサイクラーを用い、Maxモードで反応した。温度条件を以下に示した。
<PCR反応温度条件>
95℃ 10分間
(94℃30秒、68℃30秒、72℃30秒)×35サイクル
4℃ 反応終了
反応後の反応液100μlに以下のバッファー溶液を加え200μlとした。
その後、この溶液200μlを専用チャンバーに入れ(http://www.mrc.co.jp/genome/about/usage.htmlに記載)、引き続いてDNAマイクロアレイを入れてふたを閉め、55℃で2時間インキュベートした。
インキュベート後、チップをそれぞれ0.24M TNT buffer 10mlに55℃、20分間浸漬した。その後、引き続いて、0.24M TN buffer 10mlに55℃、10分間浸漬して洗浄を実施した。洗浄後、検出を実施した。
検出は、冷却CCDカメラ方式のDNAマイクロアレイ自動検出装置を用いた。DNAマイクロアレイをウェル上部から露光時間4秒間で撮像し、各スポットにおけるcy5の蛍光シグナルを検出した。マイクロアレイ上のプローブが搭載されていないスポットをブランクスポットとし、その蛍光強度の中央値をバックグラウンド値とした。すべてのスポットの蛍光強度からバックグランド値を減算した値を各プローブのシグナルとした。
結果を表6にしめした。
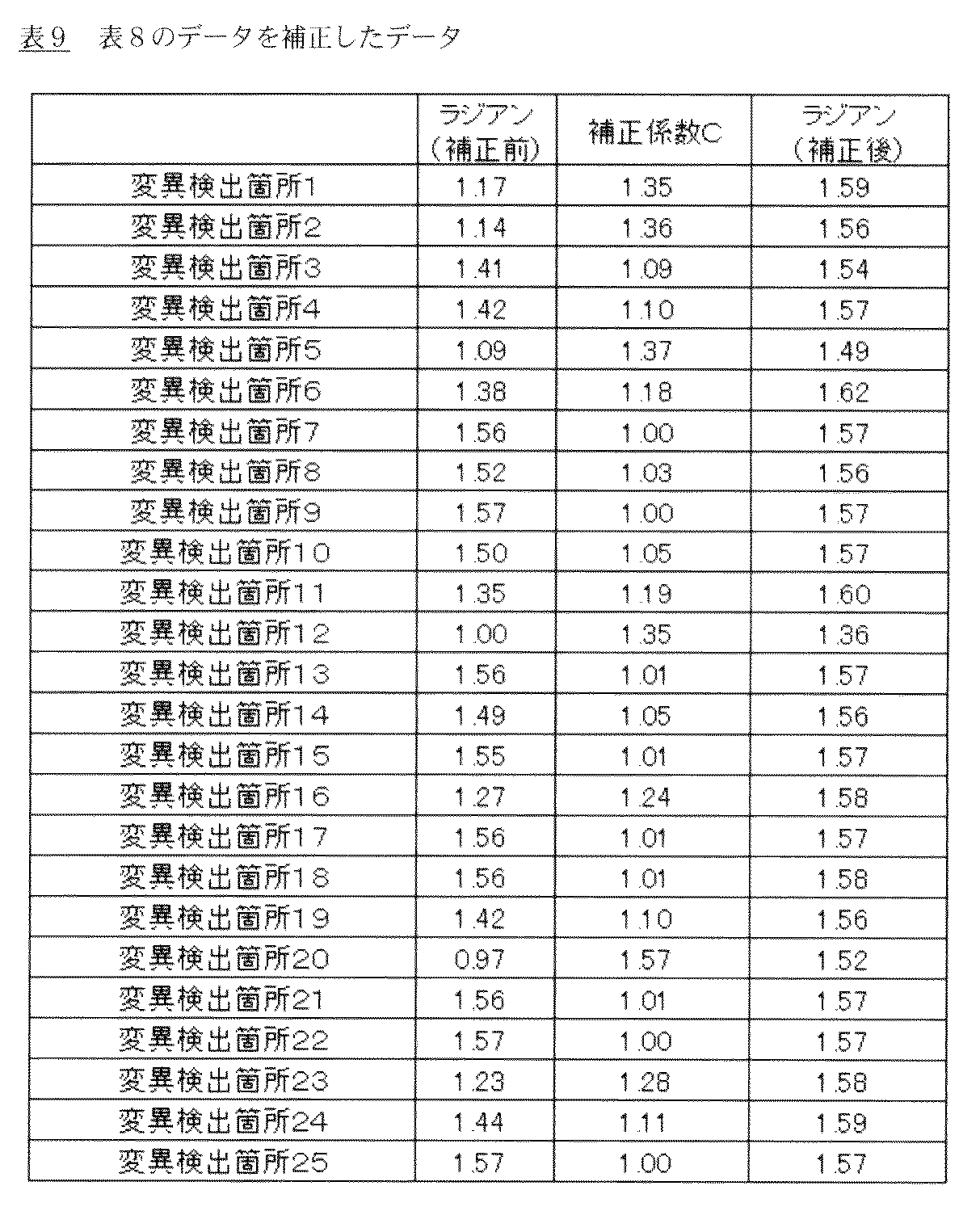
その後、誤差範囲として、野生型24データの標準偏差に補正値C、または補正値C2を乗算することにより、補正後の誤差範囲を算出した(表7右端)。
誤差範囲の上端または下端を遺伝子型の判定の範囲として補正前後でのデータについて図9(図9プラスミド由来の25種類のサンプルから得られたデータの補正前、補正後)に示した。
引き続き、表8のシグナル強度をプローブペアごとに(野生型プローブに由来するシグナル)/(変異型プローブに由来するシグナル)を算出した後、ラジアン単位に換算し、さらに表7中の補正値Cを乗算した。結果を表9に示した。また図9の補正後のグラフに表9のデータを重ね合わせたところ(図10:図9の補正後のグラフに表9のデータを重ね合わせた結果)、変異箇所12番のところのみ、野生型のエラーバーと変異型のエラーバーで示される間にプロットされ、ヘテロ接合であることが判定できた。
配列番号21~24:プライマー
配列番号25~66:プローブ
配列表
Claims (20)
- 1以上の多型を有するポリヌクレオチド配列を検出するためのプローブであって、
当該配列とハイブリダイズし、且つ、少なくとも以下の要件のいずれか1つを満たすことを特徴とする、プローブ。
(1)当該配列の両端に、それぞれ1つ以上の非相補的な塩基が含まれること
(2)当該配列中に含まれる複数の多型のうち、検出目的ではない多型と対応する部分がユニバーサル塩基であること
(3)検出目的の多型が、プローブのいずれかの末端から6塩基以下の位置にあること - 1以上の多型を有するポリヌクレオチド配列が、当該配列中グアニン及びシトシンの含有量の合計が63%以上の配列であって、
当該配列とハイブリダイズし、且つ、以下の(1)及び/又は(2)の要件を満たすことを特徴とする、プローブ。
(1)当該配列の両端に、それぞれ1つ以上の非相補的な塩基が含まれること
(2)当該配列中に含まれる複数の多型のうち、検出目的ではない多型と対応する部分がユニバーサル塩基であること - 1以上の多型を有するポリヌクレオチド配列が、当該配列中グアニン及びシトシンの含有量の合計が45%以下の配列であって、
当該配列とハイブリダイズし、且つ、
検出目的の多型が、プローブのいずれかの末端から6塩基以下の位置にあること、
を特徴とする、プローブ。 - 1以上の多型を有するポリヌクレオチド配列がヒトβグロビン遺伝子配列である、請求項1~3のいずれかに記載のプローブ。
- グアニン及びシトシンの含有量の合計が63%以上である、1以上の多型を有するポリヌクレオチド配列が、配列番号3、4、7、8、17又は18に記載の配列を有する、請求項2記載のプローブ。
- グアニン及びシトシンの含有量の合計が45%以下である、1以上の多型を有するポリヌクレオチド配列が、配列番号11又は12に記載の配列を有する、請求項3記載のプローブ。
- 配列番号3、4、7、8、11、12、17又は18に記載の配列の少なくとも1つを有する、マイクロアレイ。
- 配列番号3、4、7、8、11、12、17、18、25~66に示される遺伝子を含む、βグロビン遺伝子の変異を検出するためのプローブ群。
- 配列番号3、4、7、8、11、12、17、18、25~66に記載の配列の少なくとも1つを有する、マイクロアレイ。
- 少なくとも請求項1~9のいずれか一項に記載のプローブを含む、βサラセミア検出キット。
- 請求項7、9に記載のマイクロアレイを含む、βサラセミア検出キット。
- (イ)(i)配列番号21で示されるオリゴヌクレオチドプライマーと配列番号22で示されるオリゴヌクレオチドプライマー、及び/又は(ii)配列番号23で示されるオリゴヌクレオチドプライマーと配列番号24で示されるオリゴヌクレオチドプライマーと、
(ロ)請求項7又は9に記載のマイクロアレイと
を含む、βグロビン遺伝子変異検出用キット。 - 以下の工程を含む、多型検出用マイクロアレイプローブペアの評価方法。
(1) 第1の多型検出用プローブがハイブリダイズして得られるシグナル強度を表すY軸と、第2の多型検出用プローブがハイブリダイズして得られるシグナル強度を表すX軸とを含む蛍光座標系において、第1の多型用コントロール核酸を多型検出用プローブペアとハイブリダイズして得られた蛍光座標をプロットする工程、
(2) 前記Y軸とX軸との交点Oと、前記工程(1)でプロットされた蛍光座標とを通る直線の傾きに反比例する値を補正値Cと定める工程、
(3) 工程(1)及び(2)を複数の多型検出用プローブペアについて行い、各プローブ間で補正値Cを比較し、補正値Cが最小となるプローブペアを第一の多型検出に適したプローブとして決定する工程 - 前記蛍光座標系は前記Y軸とX軸とが直交しているものである、請求項13に記載の方法。
- 前記工程(1)は、前記コントロール核酸と、前記プローブとのハイブリダイズを2回以上行って2点以上の蛍光座標を獲得し、各座標の代表値Mを定めるものであり、かつ、
前記工程(2)において、前記直線は前記交点Oと前記代表値Mとを通る中央直線である、請求項13又は14に記載の方法 - 前記工程(1)はさらに、交点Oと前記2点以上の蛍光座標とを通る複数の直線のうち、前記中央直線との傾きの差がある直線を選択し、これを誤差直線と定める処理を含み、
前記工程(2)は、
(a)前記中央直線とX軸との間の角度α(ラジアン)から、
補正値C=π/2÷αを求める処理、
(b)前記中央直線と誤差直線とがなす角度を誤差角θ(ラジアン)から、
補正誤差角θ’(ラジアン)=θ(ラジアン)×補正値C
を求める処理、
を含むものである、
請求項14又は15に記載の方法。 - 以下の工程をさらに含む、請求項13~16に記載の方法。
(4) 第2の多型用コントロール核酸を第2の多型検出用プローブペアとハイブリダイズして得られた蛍光座標をプロットする工程、
(5) 交点Oと、前記工程(4)でプロットされた蛍光座標とを通る直線の傾きに比例する値を補正値C2と定める工程、
(6) 工程(4)及び(5)を複数の第2の多型検出用プローブペアについて行い、各プローブ間で補正値C2を比較し、補正値C2が最小となるプローブペアを第2の多型検出に適したプローブとして決定する工程 - 前記工程(4)は、前記第2の多型用コントロール核酸と、前記第2の多型検出用プローブとのハイブリダイズを2回以上行って2点以上の蛍光座標を獲得し、各座標の代表値M2を定めるものであり、かつ、
前記工程(5)において、前記直線が前記交点Oと前記代表値M2とを通る第2の中央直線である、請求項17に記載の方法。 - 前記工程(4)はさらに、交点Oと前記2点以上の蛍光座標とを通る複数の直線のうち、前記第2の中央直線との傾きの差がある直線を選択し、これを誤差直線と定める処理を含み、
前記工程(5)は、
(c)前記第2の中央直線とY軸との間の角度β(ラジアン)から、
補正値C2=π/2÷βを求める処理、及び
(d)前記第2の中央直線と誤差直線とがなす角度を第2の誤差角θ2(ラジアン)から、
第2の補正誤差角θ2’(ラジアン)=θ2(ラジアン)×補正値C2
を求める処理、
を含むものである、
請求項18に記載の方法。 - 請求項13~19のいずれか一項に記載の方法を利用した遺伝子型判別表示プログラム。
Priority Applications (6)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| JP2013518900A JP6269059B2 (ja) | 2012-03-29 | 2013-03-28 | βグロビン遺伝子の変異を検出するためのマイクロアレイ及びその検出方法 |
| US14/384,116 US20150184241A1 (en) | 2012-03-29 | 2013-03-28 | MICROARRAY FOR DETECTION OF MUTATIONS IN beta-GLOBIN GENES AND DETECTION METHOD THEREOF |
| EP13768660.6A EP2832863A4 (en) | 2012-03-29 | 2013-03-28 | MICROARRAY FOR THE DETECTION OF MUTATIONS IN BETA-GLOBIN GENES AND PROOF PROCESS THEREFOR |
| SG11201406010QA SG11201406010QA (en) | 2012-03-29 | 2013-03-28 | MICROARRAY FOR DETECTION OF MUTATIONS IN β-GLOBIN GENES AND DETECTION METHOD THEREOF |
| CN201380017558.4A CN104204227B (zh) | 2012-03-29 | 2013-03-28 | 用于检测β球蛋白基因的变异的微阵列及其检测方法 |
| US15/998,496 US20190040468A1 (en) | 2012-03-29 | 2018-08-16 | Microarray for detection of mutations in beta-globin genes and detection method thereof |
Applications Claiming Priority (2)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| JP2012-077394 | 2012-03-29 | ||
| JP2012077394 | 2012-03-29 |
Related Child Applications (2)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| US14/384,116 A-371-Of-International US20150184241A1 (en) | 2012-03-29 | 2013-03-28 | MICROARRAY FOR DETECTION OF MUTATIONS IN beta-GLOBIN GENES AND DETECTION METHOD THEREOF |
| US15/998,496 Division US20190040468A1 (en) | 2012-03-29 | 2018-08-16 | Microarray for detection of mutations in beta-globin genes and detection method thereof |
Publications (1)
| Publication Number | Publication Date |
|---|---|
| WO2013147320A1 true WO2013147320A1 (ja) | 2013-10-03 |
Family
ID=49260550
Family Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| PCT/JP2013/060261 WO2013147320A1 (ja) | 2012-03-29 | 2013-03-28 | βグロビン遺伝子の変異を検出するためのマイクロアレイ及びその検出方法 |
Country Status (7)
| Country | Link |
|---|---|
| US (2) | US20150184241A1 (ja) |
| EP (2) | EP3138928A1 (ja) |
| JP (2) | JP6269059B2 (ja) |
| CN (3) | CN105969848A (ja) |
| SG (2) | SG11201406010QA (ja) |
| TW (2) | TWI582105B (ja) |
| WO (1) | WO2013147320A1 (ja) |
Cited By (1)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| CN111733232A (zh) * | 2020-07-02 | 2020-10-02 | 南京艾迪康医学检验所有限公司 | 检测hbb基因突变的引物、方法和试剂盒 |
Families Citing this family (6)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| WO2019022018A1 (ja) * | 2017-07-24 | 2019-01-31 | 国立研究開発法人農業・食品産業技術総合研究機構 | 多型検出法 |
| CN109490811B (zh) * | 2018-11-23 | 2021-08-13 | 国网四川省电力公司 | 一种倒立式电流互感器的油压监测方法 |
| CN111321211A (zh) * | 2018-12-14 | 2020-06-23 | 北京大学深圳医院 | 人β地中海贫血基因分型检测的试剂及检测方法 |
| CN110093413A (zh) * | 2019-04-09 | 2019-08-06 | 深圳市卫生健康发展研究中心 | 检测β地中海贫血的引物组和试剂盒 |
| CN112646872A (zh) * | 2020-11-24 | 2021-04-13 | 阅尔基因技术(苏州)有限公司 | 一种检测α-地贫和β-地贫点突变的方法 |
| WO2023283838A1 (zh) * | 2021-07-14 | 2023-01-19 | 天津华大医学检验所有限公司 | 用于镰刀型细胞贫血症检测的组合物、试剂盒及应用 |
Citations (6)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| JPH11108928A (ja) | 1997-10-01 | 1999-04-23 | Dainakomu:Kk | 生体高分子配列シートの製造方法 |
| JP2000189199A (ja) * | 1986-03-13 | 2000-07-11 | F Hoffmann La Roche Ag | 特定のヌクレオチド配列の検出方法及びキット |
| JP2001133453A (ja) | 1999-08-26 | 2001-05-18 | Mitsubishi Rayon Co Ltd | 生体高分子配列薄片の製造方法 |
| WO2002062817A1 (fr) | 2001-02-08 | 2002-08-15 | Mitsubishi Rayon Co., Ltd. | Procede de production d'acide nucleique vinyle |
| JP2005000127A (ja) * | 2003-06-13 | 2005-01-06 | Hitachi Software Eng Co Ltd | 多型検出方法 |
| WO2006033484A1 (ja) * | 2004-09-24 | 2006-03-30 | Kyushu University, National University Corporation | 核酸マイクロアレイ及び核酸プローブの設計方法並びに遺伝子検出方法 |
Family Cites Families (21)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| US5220004A (en) * | 1991-05-07 | 1993-06-15 | Cetus Corporation | Methods and reagents for G -65 -globin typing |
| FR2749308B1 (fr) * | 1996-06-03 | 1998-07-24 | Bio Merieux | Sondes nucleotidiques et procede pour determiner le typage hla dqb1 |
| CA2369524A1 (en) * | 1999-04-27 | 2000-11-02 | University Of Chicago | Nucleotide extension on a microarray of gel-immobilized primers |
| US7013221B1 (en) * | 1999-07-16 | 2006-03-14 | Rosetta Inpharmatics Llc | Iterative probe design and detailed expression profiling with flexible in-situ synthesis arrays |
| US20030096986A1 (en) * | 2001-10-25 | 2003-05-22 | Affymetrix, Incorporated | Methods and computer software products for selecting nucleic acid probes |
| US7858301B2 (en) * | 2003-05-07 | 2010-12-28 | Bioarray Solutions, Ltd. | Method of probe design for nucleic acid analysis by multiplexed hybridization |
| WO2004104172A2 (en) * | 2003-05-15 | 2004-12-02 | Bioarray Solutions, Ltd. | Hybridization-mediated analysis of polymorphisms |
| WO2005001091A1 (ja) * | 2003-06-27 | 2005-01-06 | Olympus Corporation | 核酸の変異及び多型の検出用プローブセット、それを固相化したdnaアレイ、並びにそれらを用いた変異及び多型の検出方法 |
| ITRM20040081A1 (it) * | 2004-02-13 | 2004-05-13 | Biochemical Systems Internat | Sonde oligonucleotidiche per la diagnosi delle diverse forme di beta-talassemia e relativi metodi e kit diagnostici. |
| US7374927B2 (en) * | 2004-05-03 | 2008-05-20 | Affymetrix, Inc. | Methods of analysis of degraded nucleic acid samples |
| US20050282174A1 (en) * | 2004-06-19 | 2005-12-22 | Webb Peter G | Methods and systems for selecting nucleic acid probes for microarrays |
| EP1778876A2 (en) * | 2004-06-30 | 2007-05-02 | Applera Corporation | Controls for determining reaction performance in polynucleotide sequence detection assays |
| AU2005286084C1 (en) * | 2004-09-24 | 2011-11-24 | Ingeneus Inc. | Genomic assay |
| US20060110744A1 (en) * | 2004-11-23 | 2006-05-25 | Sampas Nicolas M | Probe design methods and microarrays for comparative genomic hybridization and location analysis |
| KR101063037B1 (ko) * | 2005-12-08 | 2011-09-07 | 세키스이 메디칼 가부시키가이샤 | 핵산 증폭법을 이용한 인간 유두종 바이러스의 검출 방법및 핵산쇄 고정화 담체 |
| CN101336301A (zh) * | 2006-01-05 | 2008-12-31 | 西蒙斯单倍体有限公司 | 微阵列方法 |
| EP1956097A1 (en) * | 2007-02-06 | 2008-08-13 | bioMerieux B.V. | Method for discriminating single nucleotide polymorphisms (SNPs) |
| CN101354344A (zh) * | 2007-07-27 | 2009-01-28 | 上海主健生物工程有限公司 | 遗传信息及健康评估管理 |
| US20110212991A1 (en) * | 2007-09-11 | 2011-09-01 | Roche Molecular Systems, Inc. | Diagnostic Test for Susceptibility to B-RAF Kinase Inhibitors |
| CN102220411A (zh) * | 2010-04-16 | 2011-10-19 | 中山大学达安基因股份有限公司 | 一种一体化检测α、β突变型地中海贫血的试剂盒 |
| CN102277419B (zh) * | 2011-04-06 | 2012-11-21 | 广东省妇幼保健院 | 基于液相芯片系统诊断地中海贫血的方法及试剂盒与应用 |
-
2013
- 2013-03-28 CN CN201610306087.4A patent/CN105969848A/zh not_active Withdrawn
- 2013-03-28 SG SG11201406010QA patent/SG11201406010QA/en unknown
- 2013-03-28 CN CN201510428094.7A patent/CN105069324B/zh not_active Expired - Fee Related
- 2013-03-28 JP JP2013518900A patent/JP6269059B2/ja not_active Expired - Fee Related
- 2013-03-28 SG SG10201601806TA patent/SG10201601806TA/en unknown
- 2013-03-28 WO PCT/JP2013/060261 patent/WO2013147320A1/ja active Application Filing
- 2013-03-28 EP EP16192136.6A patent/EP3138928A1/en not_active Withdrawn
- 2013-03-28 EP EP13768660.6A patent/EP2832863A4/en not_active Withdrawn
- 2013-03-28 CN CN201380017558.4A patent/CN104204227B/zh not_active Expired - Fee Related
- 2013-03-28 US US14/384,116 patent/US20150184241A1/en not_active Abandoned
- 2013-03-29 TW TW102111284A patent/TWI582105B/zh not_active IP Right Cessation
- 2013-03-29 TW TW105103897A patent/TWI619723B/zh not_active IP Right Cessation
-
2016
- 2016-08-09 JP JP2016156804A patent/JP6269746B2/ja not_active Expired - Fee Related
-
2018
- 2018-08-16 US US15/998,496 patent/US20190040468A1/en not_active Abandoned
Patent Citations (6)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| JP2000189199A (ja) * | 1986-03-13 | 2000-07-11 | F Hoffmann La Roche Ag | 特定のヌクレオチド配列の検出方法及びキット |
| JPH11108928A (ja) | 1997-10-01 | 1999-04-23 | Dainakomu:Kk | 生体高分子配列シートの製造方法 |
| JP2001133453A (ja) | 1999-08-26 | 2001-05-18 | Mitsubishi Rayon Co Ltd | 生体高分子配列薄片の製造方法 |
| WO2002062817A1 (fr) | 2001-02-08 | 2002-08-15 | Mitsubishi Rayon Co., Ltd. | Procede de production d'acide nucleique vinyle |
| JP2005000127A (ja) * | 2003-06-13 | 2005-01-06 | Hitachi Software Eng Co Ltd | 多型検出方法 |
| WO2006033484A1 (ja) * | 2004-09-24 | 2006-03-30 | Kyushu University, National University Corporation | 核酸マイクロアレイ及び核酸プローブの設計方法並びに遺伝子検出方法 |
Non-Patent Citations (10)
| Title |
|---|
| AM. J. HUM. GENET., vol. 43, 1988, pages 095 - 100 |
| BLOOD, vol. 81, no. 1, 1 January 1993 (1993-01-01), pages 239 - 242 |
| ERLICH ET AL.: "Current Communications in Molecular Biology: Polymerase Chain Reaction", 1989, COLD SPRING HARBOR PRESS |
| GREGG L. SEMENZA ET AL.: "Detection of a novel DNA polymorphism in the beta-globin gene cluster.", THE JOURNAL OF BIOLOGICAL CHEMISTRY, vol. 259, no. 10, 25 May 1984 (1984-05-25), pages 6045 - 6048, XP055162949 * |
| INNIS ET AL.: "PCR Protocols: A Guide to Methods and Applications", 1990, ACADEMIC PRESS |
| JESPER PETERSENA ET AL.: "Detection of mutations in the P-globin gene by colorimetric staining of DNA microarrays visualized by a flatbed scanner.", ANALYTICAL BIOCHEMISTRY, vol. 360, no. 1, 2007, pages 169 - 171, XP005725323 * |
| MANIATIS ET AL.: "Molecular Cloning: A Laboratory Manual", 1982, COLD SPRING HARBOR, pages: 280,281 |
| SAMBROOK ET AL.: "Molecular Cloning: A Laboratory Manual, 2nd Edition,", 1989, COLD SPRING HARBOR PRESS |
| See also references of EP2832863A4 |
| WEATHERALL ET AL.: "The Thalassaemia Syndromes, 3rd Edition,", 1981, OXFORD BLACKWELL SCIENTIFIC |
Cited By (1)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| CN111733232A (zh) * | 2020-07-02 | 2020-10-02 | 南京艾迪康医学检验所有限公司 | 检测hbb基因突变的引物、方法和试剂盒 |
Also Published As
| Publication number | Publication date |
|---|---|
| CN105969848A (zh) | 2016-09-28 |
| EP3138928A1 (en) | 2017-03-08 |
| EP2832863A4 (en) | 2016-02-24 |
| CN104204227A (zh) | 2014-12-10 |
| TWI582105B (zh) | 2017-05-11 |
| JPWO2013147320A1 (ja) | 2015-12-14 |
| TWI619723B (zh) | 2018-04-01 |
| JP6269059B2 (ja) | 2018-01-31 |
| SG10201601806TA (en) | 2016-04-28 |
| TW201345919A (zh) | 2013-11-16 |
| CN104204227B (zh) | 2016-09-07 |
| US20190040468A1 (en) | 2019-02-07 |
| JP2017045451A (ja) | 2017-03-02 |
| TW201619182A (zh) | 2016-06-01 |
| US20150184241A1 (en) | 2015-07-02 |
| SG11201406010QA (en) | 2014-11-27 |
| CN105069324A (zh) | 2015-11-18 |
| EP2832863A1 (en) | 2015-02-04 |
| JP6269746B2 (ja) | 2018-01-31 |
| CN105069324B (zh) | 2018-08-28 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| JP6269746B2 (ja) | βグロビン遺伝子の変異を検出するためのマイクロアレイ及びその検出方法 | |
| JP5986572B2 (ja) | 固定化プライマーを使用した標的dnaの直接的な捕捉、増幅、および配列決定 | |
| JP2009171969A (ja) | マイクロアレイハイブリダイゼーションアッセイ方法 | |
| JP6020164B2 (ja) | 核酸の検出方法 | |
| US11667957B2 (en) | Methods and compositions for identifying ligands on arrays using indexes and barcodes | |
| JP4794832B2 (ja) | 核酸検出用プローブセット及び担体 | |
| CN113840923A (zh) | 用于核酸检测的方法、系统和设备 | |
| JPWO2007055255A1 (ja) | 複数の識別用核酸配列を増幅する方法 | |
| RU2539733C2 (ru) | Набор дифференцирующих нуклеотидов и биочип для применения в способе генотипирования маркеров гаплогрупп y-хромосомы человека: m130 (c), м145 (de) | |
| CN109415759B (zh) | 用于产生dna探针的方法以及使用dna探针分析基因组dna的方法 | |
| JP5197661B2 (ja) | 核酸検出用プローブ担体 | |
| RU2643333C1 (ru) | Способ анализа полиморфных маркеров в генах метаболизма лекарственных препаратов и генах иммунного ответа при терапии острых лейкозов у детей | |
| Tabone | Mutations, structural variations, and genome‐wide resequencing: where to from here in our understanding of disease and evolution? | |
| WO2020225564A1 (en) | Combined solution phase and solid phase dna amplification | |
| JP2007330136A (ja) | 塩基多型の同定方法 |
Legal Events
| Date | Code | Title | Description |
|---|---|---|---|
| ENP | Entry into the national phase |
Ref document number: 2013518900 Country of ref document: JP Kind code of ref document: A |
|
| 121 | Ep: the epo has been informed by wipo that ep was designated in this application |
Ref document number: 13768660 Country of ref document: EP Kind code of ref document: A1 |
|
| WWE | Wipo information: entry into national phase |
Ref document number: 14384116 Country of ref document: US |
|
| REEP | Request for entry into the european phase |
Ref document number: 2013768660 Country of ref document: EP |
|
| WWE | Wipo information: entry into national phase |
Ref document number: 2013768660 Country of ref document: EP |
|
| NENP | Non-entry into the national phase |
Ref country code: DE |