JP5798926B2 - 配列解析によって病態をモニターする方法 - Google Patents
配列解析によって病態をモニターする方法 Download PDFInfo
- Publication number
- JP5798926B2 JP5798926B2 JP2011535569A JP2011535569A JP5798926B2 JP 5798926 B2 JP5798926 B2 JP 5798926B2 JP 2011535569 A JP2011535569 A JP 2011535569A JP 2011535569 A JP2011535569 A JP 2011535569A JP 5798926 B2 JP5798926 B2 JP 5798926B2
- Authority
- JP
- Japan
- Prior art keywords
- cells
- disease
- clonal
- correlated
- sample
- Prior art date
- Legal status (The legal status is an assumption and is not a legal conclusion. Google has not performed a legal analysis and makes no representation as to the accuracy of the status listed.)
- Active
Links
- 208000037265 diseases, disorders, signs and symptoms Diseases 0.000 title description 250
- 201000010099 disease Diseases 0.000 title description 244
- 238000012300 Sequence Analysis Methods 0.000 title description 2
- 238000000034 method Methods 0.000 claims description 281
- 230000003321 amplification Effects 0.000 claims description 170
- 238000003199 nucleic acid amplification method Methods 0.000 claims description 170
- 238000012163 sequencing technique Methods 0.000 claims description 159
- 210000001744 T-lymphocyte Anatomy 0.000 claims description 119
- 210000003719 b-lymphocyte Anatomy 0.000 claims description 106
- 210000004369 blood Anatomy 0.000 claims description 103
- 239000008280 blood Substances 0.000 claims description 103
- 238000003752 polymerase chain reaction Methods 0.000 claims description 95
- 108091008874 T cell receptors Proteins 0.000 claims description 79
- 102000016266 T-Cell Antigen Receptors Human genes 0.000 claims description 75
- 150000007523 nucleic acids Chemical class 0.000 claims description 63
- 102000039446 nucleic acids Human genes 0.000 claims description 57
- 108020004707 nucleic acids Proteins 0.000 claims description 57
- 108091008875 B cell receptors Proteins 0.000 claims description 54
- 239000002773 nucleotide Substances 0.000 claims description 45
- 125000003729 nucleotide group Chemical group 0.000 claims description 45
- 238000012544 monitoring process Methods 0.000 claims description 33
- 108010047041 Complementarity Determining Regions Proteins 0.000 claims description 31
- 108700005091 Immunoglobulin Genes Proteins 0.000 claims description 16
- 108700042075 T-Cell Receptor Genes Proteins 0.000 claims description 15
- 230000015572 biosynthetic process Effects 0.000 claims description 13
- 230000002441 reversible effect Effects 0.000 claims description 6
- 238000003786 synthesis reaction Methods 0.000 claims description 3
- 101100112922 Candida albicans CDR3 gene Proteins 0.000 claims 4
- 230000002596 correlated effect Effects 0.000 description 291
- 239000000523 sample Substances 0.000 description 192
- 238000012360 testing method Methods 0.000 description 164
- 238000004422 calculation algorithm Methods 0.000 description 148
- 210000004027 cell Anatomy 0.000 description 140
- 238000011282 treatment Methods 0.000 description 129
- 230000009266 disease activity Effects 0.000 description 115
- 108020004414 DNA Proteins 0.000 description 106
- 206010028980 Neoplasm Diseases 0.000 description 94
- 239000002299 complementary DNA Substances 0.000 description 64
- 239000003814 drug Substances 0.000 description 64
- 229940079593 drug Drugs 0.000 description 62
- 208000024891 symptom Diseases 0.000 description 59
- 238000004458 analytical method Methods 0.000 description 57
- 201000006417 multiple sclerosis Diseases 0.000 description 56
- 201000000596 systemic lupus erythematosus Diseases 0.000 description 55
- 238000006243 chemical reaction Methods 0.000 description 54
- 108091032973 (ribonucleotides)n+m Proteins 0.000 description 53
- 108090000623 proteins and genes Proteins 0.000 description 47
- 230000000295 complement effect Effects 0.000 description 46
- 239000000427 antigen Substances 0.000 description 42
- 108091007433 antigens Proteins 0.000 description 42
- 102000036639 antigens Human genes 0.000 description 42
- 101100395211 Trichoderma harzianum his3 gene Proteins 0.000 description 41
- 108020004511 Recombinant DNA Proteins 0.000 description 40
- 102000004169 proteins and genes Human genes 0.000 description 40
- 208000015181 infectious disease Diseases 0.000 description 39
- 208000023275 Autoimmune disease Diseases 0.000 description 38
- DDRJAANPRJIHGJ-UHFFFAOYSA-N creatinine Chemical compound CN1CC(=O)NC1=N DDRJAANPRJIHGJ-UHFFFAOYSA-N 0.000 description 38
- 238000001514 detection method Methods 0.000 description 37
- 201000011510 cancer Diseases 0.000 description 36
- 235000018102 proteins Nutrition 0.000 description 34
- 210000001519 tissue Anatomy 0.000 description 34
- 238000001574 biopsy Methods 0.000 description 32
- 238000013459 approach Methods 0.000 description 30
- 241000282414 Homo sapiens Species 0.000 description 28
- 239000012634 fragment Substances 0.000 description 28
- 210000000987 immune system Anatomy 0.000 description 28
- 230000008859 change Effects 0.000 description 27
- 206010039073 rheumatoid arthritis Diseases 0.000 description 27
- 206010020751 Hypersensitivity Diseases 0.000 description 26
- 239000003550 marker Substances 0.000 description 26
- 230000004044 response Effects 0.000 description 25
- 230000035945 sensitivity Effects 0.000 description 25
- 230000000694 effects Effects 0.000 description 24
- 206010069754 Acquired gene mutation Diseases 0.000 description 21
- 230000001965 increasing effect Effects 0.000 description 21
- 206010036807 progressive multifocal leukoencephalopathy Diseases 0.000 description 21
- 230000037439 somatic mutation Effects 0.000 description 21
- 239000011324 bead Substances 0.000 description 20
- 229940109239 creatinine Drugs 0.000 description 19
- 238000002054 transplantation Methods 0.000 description 19
- 150000001413 amino acids Chemical group 0.000 description 18
- 230000006378 damage Effects 0.000 description 18
- 230000014509 gene expression Effects 0.000 description 18
- 230000028993 immune response Effects 0.000 description 18
- 230000004054 inflammatory process Effects 0.000 description 18
- 210000000056 organ Anatomy 0.000 description 18
- 230000008569 process Effects 0.000 description 18
- 150000003431 steroids Chemical class 0.000 description 18
- 210000002700 urine Anatomy 0.000 description 18
- 239000013566 allergen Substances 0.000 description 17
- 230000007774 longterm Effects 0.000 description 17
- 230000002829 reductive effect Effects 0.000 description 17
- 238000012549 training Methods 0.000 description 17
- 108700028369 Alleles Proteins 0.000 description 16
- 241000699666 Mus <mouse, genus> Species 0.000 description 16
- 108091028043 Nucleic acid sequence Proteins 0.000 description 16
- 230000001154 acute effect Effects 0.000 description 16
- 206010016256 fatigue Diseases 0.000 description 16
- 238000009396 hybridization Methods 0.000 description 16
- 239000000463 material Substances 0.000 description 16
- 108091093088 Amplicon Proteins 0.000 description 15
- 241000894006 Bacteria Species 0.000 description 15
- 206010061218 Inflammation Diseases 0.000 description 15
- 108091034117 Oligonucleotide Proteins 0.000 description 15
- 230000003907 kidney function Effects 0.000 description 15
- 230000007420 reactivation Effects 0.000 description 15
- 238000003753 real-time PCR Methods 0.000 description 15
- 210000001503 joint Anatomy 0.000 description 14
- 210000004698 lymphocyte Anatomy 0.000 description 14
- 238000002595 magnetic resonance imaging Methods 0.000 description 14
- 239000007787 solid Substances 0.000 description 14
- 108010074051 C-Reactive Protein Proteins 0.000 description 13
- 102100032752 C-reactive protein Human genes 0.000 description 13
- 102100027207 CD27 antigen Human genes 0.000 description 13
- 101000914511 Homo sapiens CD27 antigen Proteins 0.000 description 13
- 208000002193 Pain Diseases 0.000 description 13
- 238000009534 blood test Methods 0.000 description 13
- 210000001175 cerebrospinal fluid Anatomy 0.000 description 13
- 210000003734 kidney Anatomy 0.000 description 13
- 102000053602 DNA Human genes 0.000 description 12
- 238000002965 ELISA Methods 0.000 description 12
- 241000699670 Mus sp. Species 0.000 description 12
- 208000026935 allergic disease Diseases 0.000 description 12
- 230000000875 corresponding effect Effects 0.000 description 12
- 238000001943 fluorescence-activated cell sorting Methods 0.000 description 12
- 238000007901 in situ hybridization Methods 0.000 description 12
- 238000011862 kidney biopsy Methods 0.000 description 12
- 238000002493 microarray Methods 0.000 description 12
- 230000006798 recombination Effects 0.000 description 12
- 238000005215 recombination Methods 0.000 description 12
- 238000002255 vaccination Methods 0.000 description 12
- 206010002556 Ankylosing Spondylitis Diseases 0.000 description 11
- 102000004190 Enzymes Human genes 0.000 description 11
- 108090000790 Enzymes Proteins 0.000 description 11
- 108010002162 IgK Proteins 0.000 description 11
- 230000007815 allergy Effects 0.000 description 11
- 238000003745 diagnosis Methods 0.000 description 11
- 210000002865 immune cell Anatomy 0.000 description 11
- 239000012678 infectious agent Substances 0.000 description 11
- 230000036407 pain Effects 0.000 description 11
- 108090000765 processed proteins & peptides Proteins 0.000 description 11
- 210000005006 adaptive immune system Anatomy 0.000 description 10
- 210000004556 brain Anatomy 0.000 description 10
- 238000002790 cross-validation Methods 0.000 description 10
- 210000004602 germ cell Anatomy 0.000 description 10
- 230000036541 health Effects 0.000 description 10
- 206010025135 lupus erythematosus Diseases 0.000 description 10
- 241000282412 Homo Species 0.000 description 9
- 108060003951 Immunoglobulin Proteins 0.000 description 9
- 206010003246 arthritis Diseases 0.000 description 9
- 230000008901 benefit Effects 0.000 description 9
- 238000004364 calculation method Methods 0.000 description 9
- 208000029742 colonic neoplasm Diseases 0.000 description 9
- 102000018358 immunoglobulin Human genes 0.000 description 9
- 238000010348 incorporation Methods 0.000 description 9
- 230000000392 somatic effect Effects 0.000 description 9
- 206010009944 Colon cancer Diseases 0.000 description 8
- 229940123907 Disease modifying antirheumatic drug Drugs 0.000 description 8
- 208000009329 Graft vs Host Disease Diseases 0.000 description 8
- FBOZXECLQNJBKD-ZDUSSCGKSA-N L-methotrexate Chemical compound C=1N=C2N=C(N)N=C(N)C2=NC=1CN(C)C1=CC=C(C(=O)N[C@@H](CCC(O)=O)C(O)=O)C=C1 FBOZXECLQNJBKD-ZDUSSCGKSA-N 0.000 description 8
- LMEKQMALGUDUQG-UHFFFAOYSA-N azathioprine Chemical compound CN1C=NC([N+]([O-])=O)=C1SC1=NC=NC2=C1NC=N2 LMEKQMALGUDUQG-UHFFFAOYSA-N 0.000 description 8
- 239000002988 disease modifying antirheumatic drug Substances 0.000 description 8
- 238000009826 distribution Methods 0.000 description 8
- 238000002474 experimental method Methods 0.000 description 8
- 238000001502 gel electrophoresis Methods 0.000 description 8
- 208000024908 graft versus host disease Diseases 0.000 description 8
- 210000002216 heart Anatomy 0.000 description 8
- 238000002347 injection Methods 0.000 description 8
- 239000007924 injection Substances 0.000 description 8
- 229960000485 methotrexate Drugs 0.000 description 8
- 244000052769 pathogen Species 0.000 description 8
- 239000012071 phase Substances 0.000 description 8
- XOFYZVNMUHMLCC-ZPOLXVRWSA-N prednisone Chemical compound O=C1C=C[C@]2(C)[C@H]3C(=O)C[C@](C)([C@@](CC4)(O)C(=O)CO)[C@@H]4[C@@H]3CCC2=C1 XOFYZVNMUHMLCC-ZPOLXVRWSA-N 0.000 description 8
- 229960004618 prednisone Drugs 0.000 description 8
- 210000002966 serum Anatomy 0.000 description 8
- 230000004083 survival effect Effects 0.000 description 8
- 101100263837 Bovine ephemeral fever virus (strain BB7721) beta gene Proteins 0.000 description 7
- 101100316840 Enterobacteria phage P4 Beta gene Proteins 0.000 description 7
- 229920002153 Hydroxypropyl cellulose Polymers 0.000 description 7
- 238000003556 assay Methods 0.000 description 7
- 230000007423 decrease Effects 0.000 description 7
- 238000011161 development Methods 0.000 description 7
- 230000018109 developmental process Effects 0.000 description 7
- 239000007850 fluorescent dye Substances 0.000 description 7
- 230000012010 growth Effects 0.000 description 7
- 235000010977 hydroxypropyl cellulose Nutrition 0.000 description 7
- 230000003053 immunization Effects 0.000 description 7
- 239000003018 immunosuppressive agent Substances 0.000 description 7
- 238000009169 immunotherapy Methods 0.000 description 7
- 230000003902 lesion Effects 0.000 description 7
- 238000005259 measurement Methods 0.000 description 7
- 230000007246 mechanism Effects 0.000 description 7
- 230000035772 mutation Effects 0.000 description 7
- 238000011160 research Methods 0.000 description 7
- 238000000926 separation method Methods 0.000 description 7
- 208000035473 Communicable disease Diseases 0.000 description 6
- PMATZTZNYRCHOR-CGLBZJNRSA-N Cyclosporin A Chemical compound CC[C@@H]1NC(=O)[C@H]([C@H](O)[C@H](C)C\C=C\C)N(C)C(=O)[C@H](C(C)C)N(C)C(=O)[C@H](CC(C)C)N(C)C(=O)[C@H](CC(C)C)N(C)C(=O)[C@@H](C)NC(=O)[C@H](C)NC(=O)[C@H](CC(C)C)N(C)C(=O)[C@H](C(C)C)NC(=O)[C@H](CC(C)C)N(C)C(=O)CN(C)C1=O PMATZTZNYRCHOR-CGLBZJNRSA-N 0.000 description 6
- 108010036949 Cyclosporine Proteins 0.000 description 6
- 241000701022 Cytomegalovirus Species 0.000 description 6
- 238000000018 DNA microarray Methods 0.000 description 6
- UETNIIAIRMUTSM-UHFFFAOYSA-N Jacareubin Natural products CC1(C)OC2=CC3Oc4c(O)c(O)ccc4C(=O)C3C(=C2C=C1)O UETNIIAIRMUTSM-UHFFFAOYSA-N 0.000 description 6
- 238000000636 Northern blotting Methods 0.000 description 6
- 108091005461 Nucleic proteins Proteins 0.000 description 6
- 206010039085 Rhinitis allergic Diseases 0.000 description 6
- 238000002105 Southern blotting Methods 0.000 description 6
- 201000010105 allergic rhinitis Diseases 0.000 description 6
- 208000010668 atopic eczema Diseases 0.000 description 6
- 229960002170 azathioprine Drugs 0.000 description 6
- 239000000090 biomarker Substances 0.000 description 6
- 210000001124 body fluid Anatomy 0.000 description 6
- 150000001720 carbohydrates Chemical class 0.000 description 6
- 210000000349 chromosome Anatomy 0.000 description 6
- 230000001684 chronic effect Effects 0.000 description 6
- 229960001265 ciclosporin Drugs 0.000 description 6
- 230000000052 comparative effect Effects 0.000 description 6
- 230000034994 death Effects 0.000 description 6
- 231100000517 death Toxicity 0.000 description 6
- 238000010790 dilution Methods 0.000 description 6
- 239000012895 dilution Substances 0.000 description 6
- 238000010195 expression analysis Methods 0.000 description 6
- 230000006870 function Effects 0.000 description 6
- 238000012268 genome sequencing Methods 0.000 description 6
- 238000003384 imaging method Methods 0.000 description 6
- 238000002649 immunization Methods 0.000 description 6
- 238000003364 immunohistochemistry Methods 0.000 description 6
- 230000006872 improvement Effects 0.000 description 6
- 230000002757 inflammatory effect Effects 0.000 description 6
- 230000003993 interaction Effects 0.000 description 6
- 150000002632 lipids Chemical class 0.000 description 6
- 210000004185 liver Anatomy 0.000 description 6
- 230000001404 mediated effect Effects 0.000 description 6
- 238000010208 microarray analysis Methods 0.000 description 6
- 238000002264 polyacrylamide gel electrophoresis Methods 0.000 description 6
- 238000004062 sedimentation Methods 0.000 description 6
- 239000000243 solution Substances 0.000 description 6
- 201000005671 spondyloarthropathy Diseases 0.000 description 6
- 229960001940 sulfasalazine Drugs 0.000 description 6
- NCEXYHBECQHGNR-QZQOTICOSA-N sulfasalazine Chemical compound C1=C(O)C(C(=O)O)=CC(\N=N\C=2C=CC(=CC=2)S(=O)(=O)NC=2N=CC=CC=2)=C1 NCEXYHBECQHGNR-QZQOTICOSA-N 0.000 description 6
- NCEXYHBECQHGNR-UHFFFAOYSA-N sulfasalazine Natural products C1=C(O)C(C(=O)O)=CC(N=NC=2C=CC(=CC=2)S(=O)(=O)NC=2N=CC=CC=2)=C1 NCEXYHBECQHGNR-UHFFFAOYSA-N 0.000 description 6
- 230000001225 therapeutic effect Effects 0.000 description 6
- 238000001262 western blot Methods 0.000 description 6
- 206010002198 Anaphylactic reaction Diseases 0.000 description 5
- CMSMOCZEIVJLDB-UHFFFAOYSA-N Cyclophosphamide Chemical compound ClCCN(CCCl)P1(=O)NCCCO1 CMSMOCZEIVJLDB-UHFFFAOYSA-N 0.000 description 5
- 206010019233 Headaches Diseases 0.000 description 5
- 108020005187 Oligonucleotide Probes Proteins 0.000 description 5
- 108700042077 T-Cell Receptor beta Genes Proteins 0.000 description 5
- 206010052779 Transplant rejections Diseases 0.000 description 5
- 108060008682 Tumor Necrosis Factor Proteins 0.000 description 5
- 102000000852 Tumor Necrosis Factor-alpha Human genes 0.000 description 5
- 230000003044 adaptive effect Effects 0.000 description 5
- 230000000172 allergic effect Effects 0.000 description 5
- 208000030961 allergic reaction Diseases 0.000 description 5
- 230000036783 anaphylactic response Effects 0.000 description 5
- 208000003455 anaphylaxis Diseases 0.000 description 5
- 208000006673 asthma Diseases 0.000 description 5
- 238000004820 blood count Methods 0.000 description 5
- 210000001185 bone marrow Anatomy 0.000 description 5
- 239000002458 cell surface marker Substances 0.000 description 5
- 238000010586 diagram Methods 0.000 description 5
- 208000037765 diseases and disorders Diseases 0.000 description 5
- 208000035475 disorder Diseases 0.000 description 5
- 210000003743 erythrocyte Anatomy 0.000 description 5
- 231100000869 headache Toxicity 0.000 description 5
- 229940125721 immunosuppressive agent Drugs 0.000 description 5
- 230000002458 infectious effect Effects 0.000 description 5
- 206010022000 influenza Diseases 0.000 description 5
- 239000007788 liquid Substances 0.000 description 5
- 238000007403 mPCR Methods 0.000 description 5
- 239000002751 oligonucleotide probe Substances 0.000 description 5
- 238000005457 optimization Methods 0.000 description 5
- 230000009467 reduction Effects 0.000 description 5
- 238000010839 reverse transcription Methods 0.000 description 5
- 210000003491 skin Anatomy 0.000 description 5
- 238000007390 skin biopsy Methods 0.000 description 5
- 210000000278 spinal cord Anatomy 0.000 description 5
- 208000011580 syndromic disease Diseases 0.000 description 5
- 238000002560 therapeutic procedure Methods 0.000 description 5
- 229940079023 tysabri Drugs 0.000 description 5
- 239000013598 vector Substances 0.000 description 5
- 230000004584 weight gain Effects 0.000 description 5
- 235000019786 weight gain Nutrition 0.000 description 5
- 208000015943 Coeliac disease Diseases 0.000 description 4
- 206010010904 Convulsion Diseases 0.000 description 4
- VVNCNSJFMMFHPL-VKHMYHEASA-N D-penicillamine Chemical compound CC(C)(S)[C@@H](N)C(O)=O VVNCNSJFMMFHPL-VKHMYHEASA-N 0.000 description 4
- 238000001712 DNA sequencing Methods 0.000 description 4
- 108010014303 DNA-directed DNA polymerase Proteins 0.000 description 4
- 102000016928 DNA-directed DNA polymerase Human genes 0.000 description 4
- 206010012735 Diarrhoea Diseases 0.000 description 4
- 206010061818 Disease progression Diseases 0.000 description 4
- 208000010201 Exanthema Diseases 0.000 description 4
- 241000700605 Viruses Species 0.000 description 4
- 229940035676 analgesics Drugs 0.000 description 4
- 239000000730 antalgic agent Substances 0.000 description 4
- 229940124599 anti-inflammatory drug Drugs 0.000 description 4
- 230000005784 autoimmunity Effects 0.000 description 4
- 229960000074 biopharmaceutical Drugs 0.000 description 4
- 238000010276 construction Methods 0.000 description 4
- 230000005750 disease progression Effects 0.000 description 4
- 239000000839 emulsion Substances 0.000 description 4
- 238000011156 evaluation Methods 0.000 description 4
- 201000005884 exanthem Diseases 0.000 description 4
- 239000012530 fluid Substances 0.000 description 4
- 230000004927 fusion Effects 0.000 description 4
- 208000002672 hepatitis B Diseases 0.000 description 4
- 210000003630 histaminocyte Anatomy 0.000 description 4
- 229960004171 hydroxychloroquine Drugs 0.000 description 4
- XXSMGPRMXLTPCZ-UHFFFAOYSA-N hydroxychloroquine Chemical compound ClC1=CC=C2C(NC(C)CCCN(CCO)CC)=CC=NC2=C1 XXSMGPRMXLTPCZ-UHFFFAOYSA-N 0.000 description 4
- 230000009610 hypersensitivity Effects 0.000 description 4
- 238000011493 immune profiling Methods 0.000 description 4
- 230000000899 immune system response Effects 0.000 description 4
- 230000001976 improved effect Effects 0.000 description 4
- 238000000338 in vitro Methods 0.000 description 4
- 230000000977 initiatory effect Effects 0.000 description 4
- 230000002427 irreversible effect Effects 0.000 description 4
- 210000003141 lower extremity Anatomy 0.000 description 4
- 210000004072 lung Anatomy 0.000 description 4
- HPNSFSBZBAHARI-UHFFFAOYSA-N micophenolic acid Natural products OC1=C(CC=C(C)CCC(O)=O)C(OC)=C(C)C2=C1C(=O)OC2 HPNSFSBZBAHARI-UHFFFAOYSA-N 0.000 description 4
- RTGDFNSFWBGLEC-SYZQJQIISA-N mycophenolate mofetil Chemical compound COC1=C(C)C=2COC(=O)C=2C(O)=C1C\C=C(/C)CCC(=O)OCCN1CCOCC1 RTGDFNSFWBGLEC-SYZQJQIISA-N 0.000 description 4
- 229960005027 natalizumab Drugs 0.000 description 4
- 210000005036 nerve Anatomy 0.000 description 4
- 229940021182 non-steroidal anti-inflammatory drug Drugs 0.000 description 4
- 230000001717 pathogenic effect Effects 0.000 description 4
- 230000001575 pathological effect Effects 0.000 description 4
- 239000013610 patient sample Substances 0.000 description 4
- 229960001639 penicillamine Drugs 0.000 description 4
- 208000005987 polymyositis Diseases 0.000 description 4
- 102000004196 processed proteins & peptides Human genes 0.000 description 4
- 206010037844 rash Diseases 0.000 description 4
- 210000005084 renal tissue Anatomy 0.000 description 4
- 210000000952 spleen Anatomy 0.000 description 4
- 230000008961 swelling Effects 0.000 description 4
- 210000001179 synovial fluid Anatomy 0.000 description 4
- 230000009897 systematic effect Effects 0.000 description 4
- 238000012176 true single molecule sequencing Methods 0.000 description 4
- 208000027930 type IV hypersensitivity disease Diseases 0.000 description 4
- 210000001364 upper extremity Anatomy 0.000 description 4
- 238000002562 urinalysis Methods 0.000 description 4
- 229960005486 vaccine Drugs 0.000 description 4
- RZVAJINKPMORJF-UHFFFAOYSA-N Acetaminophen Chemical compound CC(=O)NC1=CC=C(O)C=C1 RZVAJINKPMORJF-UHFFFAOYSA-N 0.000 description 3
- 208000006820 Arthralgia Diseases 0.000 description 3
- 208000034048 Asymptomatic disease Diseases 0.000 description 3
- 208000008439 Biliary Liver Cirrhosis Diseases 0.000 description 3
- 208000033222 Biliary cirrhosis primary Diseases 0.000 description 3
- 108010012236 Chemokines Proteins 0.000 description 3
- 102000019034 Chemokines Human genes 0.000 description 3
- 208000017667 Chronic Disease Diseases 0.000 description 3
- 229930105110 Cyclosporin A Natural products 0.000 description 3
- 208000004262 Food Hypersensitivity Diseases 0.000 description 3
- 108010072051 Glatiramer Acetate Proteins 0.000 description 3
- 102100034343 Integrase Human genes 0.000 description 3
- 108010005714 Interferon beta-1b Proteins 0.000 description 3
- 241000701460 JC polyomavirus Species 0.000 description 3
- 208000032420 Latent Infection Diseases 0.000 description 3
- FQISKWAFAHGMGT-SGJOWKDISA-M Methylprednisolone sodium succinate Chemical compound [Na+].C([C@@]12C)=CC(=O)C=C1[C@@H](C)C[C@@H]1[C@@H]2[C@@H](O)C[C@]2(C)[C@@](O)(C(=O)COC(=O)CCC([O-])=O)CC[C@H]21 FQISKWAFAHGMGT-SGJOWKDISA-M 0.000 description 3
- 206010028813 Nausea Diseases 0.000 description 3
- 102100030569 Nuclear receptor corepressor 2 Human genes 0.000 description 3
- 101710153660 Nuclear receptor corepressor 2 Proteins 0.000 description 3
- 206010034277 Pemphigoid Diseases 0.000 description 3
- 208000012654 Primary biliary cholangitis Diseases 0.000 description 3
- 206010037660 Pyrexia Diseases 0.000 description 3
- 108010092799 RNA-directed DNA polymerase Proteins 0.000 description 3
- 206010039710 Scleroderma Diseases 0.000 description 3
- 208000021386 Sjogren Syndrome Diseases 0.000 description 3
- 108700042076 T-Cell Receptor alpha Genes Proteins 0.000 description 3
- 108010006785 Taq Polymerase Proteins 0.000 description 3
- 206010053613 Type IV hypersensitivity reaction Diseases 0.000 description 3
- 206010047700 Vomiting Diseases 0.000 description 3
- 230000001133 acceleration Effects 0.000 description 3
- 230000032683 aging Effects 0.000 description 3
- 230000003460 anti-nuclear Effects 0.000 description 3
- 208000010216 atopic IgE responsiveness Diseases 0.000 description 3
- 230000001580 bacterial effect Effects 0.000 description 3
- 229940021459 betaseron Drugs 0.000 description 3
- 230000036765 blood level Effects 0.000 description 3
- 239000010839 body fluid Substances 0.000 description 3
- 208000000594 bullous pemphigoid Diseases 0.000 description 3
- 229940107810 cellcept Drugs 0.000 description 3
- 210000003169 central nervous system Anatomy 0.000 description 3
- 238000002512 chemotherapy Methods 0.000 description 3
- 238000002591 computed tomography Methods 0.000 description 3
- 239000003246 corticosteroid Substances 0.000 description 3
- 229960004397 cyclophosphamide Drugs 0.000 description 3
- 229930182912 cyclosporin Natural products 0.000 description 3
- 201000001981 dermatomyositis Diseases 0.000 description 3
- 238000013461 design Methods 0.000 description 3
- XPPKVPWEQAFLFU-UHFFFAOYSA-J diphosphate(4-) Chemical compound [O-]P([O-])(=O)OP([O-])([O-])=O XPPKVPWEQAFLFU-UHFFFAOYSA-J 0.000 description 3
- 235000011180 diphosphates Nutrition 0.000 description 3
- 239000000428 dust Substances 0.000 description 3
- 230000008030 elimination Effects 0.000 description 3
- 238000003379 elimination reaction Methods 0.000 description 3
- 238000005516 engineering process Methods 0.000 description 3
- 235000020932 food allergy Nutrition 0.000 description 3
- 238000010166 immunofluorescence Methods 0.000 description 3
- 230000002998 immunogenetic effect Effects 0.000 description 3
- 239000002955 immunomodulating agent Substances 0.000 description 3
- 229940121354 immunomodulator Drugs 0.000 description 3
- 230000001506 immunosuppresive effect Effects 0.000 description 3
- 230000004968 inflammatory condition Effects 0.000 description 3
- 210000005007 innate immune system Anatomy 0.000 description 3
- 230000010354 integration Effects 0.000 description 3
- 238000009533 lab test Methods 0.000 description 3
- 210000000265 leukocyte Anatomy 0.000 description 3
- 238000011866 long-term treatment Methods 0.000 description 3
- 238000012423 maintenance Methods 0.000 description 3
- 206010061289 metastatic neoplasm Diseases 0.000 description 3
- 229960004866 mycophenolate mofetil Drugs 0.000 description 3
- 230000008693 nausea Effects 0.000 description 3
- 201000008383 nephritis Diseases 0.000 description 3
- 229910052757 nitrogen Inorganic materials 0.000 description 3
- 239000000041 non-steroidal anti-inflammatory agent Substances 0.000 description 3
- 230000008816 organ damage Effects 0.000 description 3
- 238000006116 polymerization reaction Methods 0.000 description 3
- 230000037452 priming Effects 0.000 description 3
- 238000004393 prognosis Methods 0.000 description 3
- 208000037821 progressive disease Diseases 0.000 description 3
- 238000012175 pyrosequencing Methods 0.000 description 3
- 230000009257 reactivity Effects 0.000 description 3
- 230000000306 recurrent effect Effects 0.000 description 3
- 229960004641 rituximab Drugs 0.000 description 3
- 210000003131 sacroiliac joint Anatomy 0.000 description 3
- 230000000405 serological effect Effects 0.000 description 3
- 230000009885 systemic effect Effects 0.000 description 3
- 238000002604 ultrasonography Methods 0.000 description 3
- 241001430294 unidentified retrovirus Species 0.000 description 3
- 238000012795 verification Methods 0.000 description 3
- 230000008673 vomiting Effects 0.000 description 3
- 208000016261 weight loss Diseases 0.000 description 3
- 230000004580 weight loss Effects 0.000 description 3
- 208000030507 AIDS Diseases 0.000 description 2
- 208000008822 Ankylosis Diseases 0.000 description 2
- 102000006306 Antigen Receptors Human genes 0.000 description 2
- 108010083359 Antigen Receptors Proteins 0.000 description 2
- BSYNRYMUTXBXSQ-UHFFFAOYSA-N Aspirin Chemical compound CC(=O)OC1=CC=CC=C1C(O)=O BSYNRYMUTXBXSQ-UHFFFAOYSA-N 0.000 description 2
- 206010003827 Autoimmune hepatitis Diseases 0.000 description 2
- 230000003844 B-cell-activation Effects 0.000 description 2
- 208000008035 Back Pain Diseases 0.000 description 2
- KPYSYYIEGFHWSV-UHFFFAOYSA-N Baclofen Chemical compound OC(=O)CC(CN)C1=CC=C(Cl)C=C1 KPYSYYIEGFHWSV-UHFFFAOYSA-N 0.000 description 2
- 208000023328 Basedow disease Diseases 0.000 description 2
- 201000004569 Blindness Diseases 0.000 description 2
- 206010008342 Cervix carcinoma Diseases 0.000 description 2
- 208000000094 Chronic Pain Diseases 0.000 description 2
- 102000004127 Cytokines Human genes 0.000 description 2
- 108090000695 Cytokines Proteins 0.000 description 2
- XUIIKFGFIJCVMT-GFCCVEGCSA-N D-thyroxine Chemical compound IC1=CC(C[C@@H](N)C(O)=O)=CC(I)=C1OC1=CC(I)=C(O)C(I)=C1 XUIIKFGFIJCVMT-GFCCVEGCSA-N 0.000 description 2
- 230000004544 DNA amplification Effects 0.000 description 2
- 208000019505 Deglutition disease Diseases 0.000 description 2
- 206010012438 Dermatitis atopic Diseases 0.000 description 2
- 108010008165 Etanercept Proteins 0.000 description 2
- 229910052688 Gadolinium Inorganic materials 0.000 description 2
- 208000034826 Genetic Predisposition to Disease Diseases 0.000 description 2
- 208000015023 Graves' disease Diseases 0.000 description 2
- 208000030836 Hashimoto thyroiditis Diseases 0.000 description 2
- 208000004044 Hypesthesia Diseases 0.000 description 2
- HEFNNWSXXWATRW-UHFFFAOYSA-N Ibuprofen Chemical compound CC(C)CC1=CC=C(C(C)C(O)=O)C=C1 HEFNNWSXXWATRW-UHFFFAOYSA-N 0.000 description 2
- 208000001718 Immediate Hypersensitivity Diseases 0.000 description 2
- 108010019476 Immunoglobulin Heavy Chains Proteins 0.000 description 2
- 108010005716 Interferon beta-1a Proteins 0.000 description 2
- 102000004889 Interleukin-6 Human genes 0.000 description 2
- 108090001005 Interleukin-6 Proteins 0.000 description 2
- 206010023230 Joint stiffness Diseases 0.000 description 2
- 208000005777 Lupus Nephritis Diseases 0.000 description 2
- 241001465754 Metazoa Species 0.000 description 2
- 208000003250 Mixed connective tissue disease Diseases 0.000 description 2
- 208000016285 Movement disease Diseases 0.000 description 2
- 208000007101 Muscle Cramp Diseases 0.000 description 2
- 208000000112 Myalgia Diseases 0.000 description 2
- 208000028389 Nerve injury Diseases 0.000 description 2
- 238000012408 PCR amplification Methods 0.000 description 2
- 206010034568 Peripheral coldness Diseases 0.000 description 2
- 208000031845 Pernicious anaemia Diseases 0.000 description 2
- 201000007100 Pharyngitis Diseases 0.000 description 2
- 206010036790 Productive cough Diseases 0.000 description 2
- 208000003251 Pruritus Diseases 0.000 description 2
- 108020004682 Single-Stranded DNA Proteins 0.000 description 2
- 208000005392 Spasm Diseases 0.000 description 2
- 208000006045 Spondylarthropathies Diseases 0.000 description 2
- 206010044565 Tremor Diseases 0.000 description 2
- 206010045240 Type I hypersensitivity Diseases 0.000 description 2
- 208000006105 Uterine Cervical Neoplasms Diseases 0.000 description 2
- 206010047115 Vasculitis Diseases 0.000 description 2
- PNNCWTXUWKENPE-UHFFFAOYSA-N [N].NC(N)=O Chemical compound [N].NC(N)=O PNNCWTXUWKENPE-UHFFFAOYSA-N 0.000 description 2
- 229960001138 acetylsalicylic acid Drugs 0.000 description 2
- 229960002964 adalimumab Drugs 0.000 description 2
- 230000006978 adaptation Effects 0.000 description 2
- 230000033289 adaptive immune response Effects 0.000 description 2
- 230000009824 affinity maturation Effects 0.000 description 2
- 239000002333 angiotensin II receptor antagonist Substances 0.000 description 2
- 229940125364 angiotensin receptor blocker Drugs 0.000 description 2
- 230000030741 antigen processing and presentation Effects 0.000 description 2
- 230000004596 appetite loss Effects 0.000 description 2
- 210000001742 aqueous humor Anatomy 0.000 description 2
- 201000008937 atopic dermatitis Diseases 0.000 description 2
- 210000003651 basophil Anatomy 0.000 description 2
- 230000009286 beneficial effect Effects 0.000 description 2
- 210000000988 bone and bone Anatomy 0.000 description 2
- 238000010322 bone marrow transplantation Methods 0.000 description 2
- 230000006931 brain damage Effects 0.000 description 2
- 231100000874 brain damage Toxicity 0.000 description 2
- 208000029028 brain injury Diseases 0.000 description 2
- 230000001413 cellular effect Effects 0.000 description 2
- 208000011235 central nervous system lupus Diseases 0.000 description 2
- 210000002939 cerumen Anatomy 0.000 description 2
- 201000010881 cervical cancer Diseases 0.000 description 2
- 210000000038 chest Anatomy 0.000 description 2
- HVYWMOMLDIMFJA-DPAQBDIFSA-N cholesterol Chemical compound C1C=C2C[C@@H](O)CC[C@]2(C)[C@@H]2[C@@H]1[C@@H]1CC[C@H]([C@H](C)CCCC(C)C)[C@@]1(C)CC2 HVYWMOMLDIMFJA-DPAQBDIFSA-N 0.000 description 2
- 201000009151 chronic rhinitis Diseases 0.000 description 2
- 230000009668 clonal growth Effects 0.000 description 2
- 210000001072 colon Anatomy 0.000 description 2
- 239000002872 contrast media Substances 0.000 description 2
- 229940038717 copaxone Drugs 0.000 description 2
- 229960001334 corticosteroids Drugs 0.000 description 2
- 230000000139 costimulatory effect Effects 0.000 description 2
- 210000001151 cytotoxic T lymphocyte Anatomy 0.000 description 2
- 230000003247 decreasing effect Effects 0.000 description 2
- 238000012217 deletion Methods 0.000 description 2
- 230000037430 deletion Effects 0.000 description 2
- 238000007847 digital PCR Methods 0.000 description 2
- 208000037771 disease arising from reactivation of latent virus Diseases 0.000 description 2
- 239000000975 dye Substances 0.000 description 2
- 230000007613 environmental effect Effects 0.000 description 2
- 229960000403 etanercept Drugs 0.000 description 2
- 230000005669 field effect Effects 0.000 description 2
- 235000013305 food Nutrition 0.000 description 2
- 238000007672 fourth generation sequencing Methods 0.000 description 2
- UIWYJDYFSGRHKR-UHFFFAOYSA-N gadolinium atom Chemical compound [Gd] UIWYJDYFSGRHKR-UHFFFAOYSA-N 0.000 description 2
- 239000000499 gel Substances 0.000 description 2
- 239000011521 glass Substances 0.000 description 2
- 150000002344 gold compounds Chemical class 0.000 description 2
- 210000002443 helper t lymphocyte Anatomy 0.000 description 2
- 238000005534 hematocrit Methods 0.000 description 2
- 238000004128 high performance liquid chromatography Methods 0.000 description 2
- 208000034783 hypoesthesia Diseases 0.000 description 2
- 230000001900 immune effect Effects 0.000 description 2
- 230000036039 immunity Effects 0.000 description 2
- 229960003444 immunosuppressant agent Drugs 0.000 description 2
- 229940073062 imuran Drugs 0.000 description 2
- 238000011534 incubation Methods 0.000 description 2
- CGIGDMFJXJATDK-UHFFFAOYSA-N indomethacin Chemical compound CC1=C(CC(O)=O)C2=CC(OC)=CC=C2N1C(=O)C1=CC=C(Cl)C=C1 CGIGDMFJXJATDK-UHFFFAOYSA-N 0.000 description 2
- 230000006749 inflammatory damage Effects 0.000 description 2
- 229960000598 infliximab Drugs 0.000 description 2
- 229940100601 interleukin-6 Drugs 0.000 description 2
- 210000002977 intracellular fluid Anatomy 0.000 description 2
- 238000007852 inverse PCR Methods 0.000 description 2
- 238000002955 isolation Methods 0.000 description 2
- 229960000681 leflunomide Drugs 0.000 description 2
- VHOGYURTWQBHIL-UHFFFAOYSA-N leflunomide Chemical compound O1N=CC(C(=O)NC=2C=CC(=CC=2)C(F)(F)F)=C1C VHOGYURTWQBHIL-UHFFFAOYSA-N 0.000 description 2
- 208000032839 leukemia Diseases 0.000 description 2
- 238000010234 longitudinal analysis Methods 0.000 description 2
- 208000019017 loss of appetite Diseases 0.000 description 2
- 235000021266 loss of appetite Nutrition 0.000 description 2
- 238000009593 lumbar puncture Methods 0.000 description 2
- 235000019689 luncheon sausage Nutrition 0.000 description 2
- 210000002540 macrophage Anatomy 0.000 description 2
- 238000002826 magnetic-activated cell sorting Methods 0.000 description 2
- 230000036210 malignancy Effects 0.000 description 2
- 238000004519 manufacturing process Methods 0.000 description 2
- 238000002844 melting Methods 0.000 description 2
- 230000008018 melting Effects 0.000 description 2
- 230000015654 memory Effects 0.000 description 2
- 230000001394 metastastic effect Effects 0.000 description 2
- 229960004584 methylprednisolone Drugs 0.000 description 2
- 239000000693 micelle Substances 0.000 description 2
- 206010063344 microscopic polyangiitis Diseases 0.000 description 2
- 230000027939 micturition Effects 0.000 description 2
- DYKFCLLONBREIL-KVUCHLLUSA-N minocycline Chemical compound C([C@H]1C2)C3=C(N(C)C)C=CC(O)=C3C(=O)C1=C(O)[C@@]1(O)[C@@H]2[C@H](N(C)C)C(O)=C(C(N)=O)C1=O DYKFCLLONBREIL-KVUCHLLUSA-N 0.000 description 2
- 229960004023 minocycline Drugs 0.000 description 2
- KKZJGLLVHKMTCM-UHFFFAOYSA-N mitoxantrone Chemical compound O=C1C2=C(O)C=CC(O)=C2C(=O)C2=C1C(NCCNCCO)=CC=C2NCCNCCO KKZJGLLVHKMTCM-UHFFFAOYSA-N 0.000 description 2
- 239000000203 mixture Substances 0.000 description 2
- 230000004048 modification Effects 0.000 description 2
- 238000012986 modification Methods 0.000 description 2
- 238000010172 mouse model Methods 0.000 description 2
- 208000013465 muscle pain Diseases 0.000 description 2
- 210000000822 natural killer cell Anatomy 0.000 description 2
- 230000008764 nerve damage Effects 0.000 description 2
- 230000000926 neurological effect Effects 0.000 description 2
- 210000000440 neutrophil Anatomy 0.000 description 2
- 231100000862 numbness Toxicity 0.000 description 2
- 229960005489 paracetamol Drugs 0.000 description 2
- 230000036961 partial effect Effects 0.000 description 2
- 210000004197 pelvis Anatomy 0.000 description 2
- 210000005259 peripheral blood Anatomy 0.000 description 2
- 239000011886 peripheral blood Substances 0.000 description 2
- 210000002381 plasma Anatomy 0.000 description 2
- 238000012123 point-of-care testing Methods 0.000 description 2
- 229920001184 polypeptide Polymers 0.000 description 2
- 230000002035 prolonged effect Effects 0.000 description 2
- 201000001474 proteinuria Diseases 0.000 description 2
- 230000005855 radiation Effects 0.000 description 2
- 108020003175 receptors Proteins 0.000 description 2
- 102000005962 receptors Human genes 0.000 description 2
- 238000002271 resection Methods 0.000 description 2
- 206010039083 rhinitis Diseases 0.000 description 2
- 238000005070 sampling Methods 0.000 description 2
- 238000012216 screening Methods 0.000 description 2
- 230000028327 secretion Effects 0.000 description 2
- 231100000046 skin rash Toxicity 0.000 description 2
- 239000007790 solid phase Substances 0.000 description 2
- 210000003802 sputum Anatomy 0.000 description 2
- 208000024794 sputum Diseases 0.000 description 2
- 238000010561 standard procedure Methods 0.000 description 2
- 239000000126 substance Substances 0.000 description 2
- 238000001356 surgical procedure Methods 0.000 description 2
- 230000002459 sustained effect Effects 0.000 description 2
- 201000004595 synovitis Diseases 0.000 description 2
- 230000009258 tissue cross reactivity Effects 0.000 description 2
- XFYDIVBRZNQMJC-UHFFFAOYSA-N tizanidine Chemical compound ClC=1C=CC2=NSN=C2C=1NC1=NCCN1 XFYDIVBRZNQMJC-UHFFFAOYSA-N 0.000 description 2
- 238000011269 treatment regimen Methods 0.000 description 2
- 230000005951 type IV hypersensitivity Effects 0.000 description 2
- 230000002485 urinary effect Effects 0.000 description 2
- 230000004393 visual impairment Effects 0.000 description 2
- VKZRWSNIWNFCIQ-WDSKDSINSA-N (2s)-2-[2-[[(1s)-1,2-dicarboxyethyl]amino]ethylamino]butanedioic acid Chemical compound OC(=O)C[C@@H](C(O)=O)NCCN[C@H](C(O)=O)CC(O)=O VKZRWSNIWNFCIQ-WDSKDSINSA-N 0.000 description 1
- 239000005541 ACE inhibitor Substances 0.000 description 1
- 208000004998 Abdominal Pain Diseases 0.000 description 1
- 208000000187 Abnormal Reflex Diseases 0.000 description 1
- 206010000171 Abnormal reflexes Diseases 0.000 description 1
- 208000026872 Addison Disease Diseases 0.000 description 1
- 206010067484 Adverse reaction Diseases 0.000 description 1
- 208000035285 Allergic Seasonal Rhinitis Diseases 0.000 description 1
- 201000004384 Alopecia Diseases 0.000 description 1
- 208000024827 Alzheimer disease Diseases 0.000 description 1
- 206010001935 American trypanosomiasis Diseases 0.000 description 1
- 206010002383 Angina Pectoris Diseases 0.000 description 1
- 208000003343 Antiphospholipid Syndrome Diseases 0.000 description 1
- 208000019901 Anxiety disease Diseases 0.000 description 1
- 206010002921 Aortitis Diseases 0.000 description 1
- 239000005552 B01AC04 - Clopidogrel Substances 0.000 description 1
- 208000035143 Bacterial infection Diseases 0.000 description 1
- 208000012639 Balance disease Diseases 0.000 description 1
- 208000009137 Behcet syndrome Diseases 0.000 description 1
- 206010051779 Bone marrow toxicity Diseases 0.000 description 1
- 102100026008 Breakpoint cluster region protein Human genes 0.000 description 1
- 206010006187 Breast cancer Diseases 0.000 description 1
- 208000026310 Breast neoplasm Diseases 0.000 description 1
- 206010051290 Central nervous system lesion Diseases 0.000 description 1
- 206010050337 Cerumen impaction Diseases 0.000 description 1
- 208000024699 Chagas disease Diseases 0.000 description 1
- 208000006545 Chronic Obstructive Pulmonary Disease Diseases 0.000 description 1
- 206010009192 Circulatory collapse Diseases 0.000 description 1
- 241000193163 Clostridioides difficile Species 0.000 description 1
- 206010010741 Conjunctivitis Diseases 0.000 description 1
- 108091035707 Consensus sequence Proteins 0.000 description 1
- 206010010774 Constipation Diseases 0.000 description 1
- 206010011409 Cross infection Diseases 0.000 description 1
- 208000014311 Cushing syndrome Diseases 0.000 description 1
- IGXWBGJHJZYPQS-SSDOTTSWSA-N D-Luciferin Chemical compound OC(=O)[C@H]1CSC(C=2SC3=CC=C(O)C=C3N=2)=N1 IGXWBGJHJZYPQS-SSDOTTSWSA-N 0.000 description 1
- -1 DNA (eg Chemical class 0.000 description 1
- 206010011878 Deafness Diseases 0.000 description 1
- CYCGRDQQIOGCKX-UHFFFAOYSA-N Dehydro-luciferin Natural products OC(=O)C1=CSC(C=2SC3=CC(O)=CC=C3N=2)=N1 CYCGRDQQIOGCKX-UHFFFAOYSA-N 0.000 description 1
- 208000006313 Delayed Hypersensitivity Diseases 0.000 description 1
- 208000016192 Demyelinating disease Diseases 0.000 description 1
- 201000004624 Dermatitis Diseases 0.000 description 1
- 206010012434 Dermatitis allergic Diseases 0.000 description 1
- 206010012442 Dermatitis contact Diseases 0.000 description 1
- 208000003164 Diplopia Diseases 0.000 description 1
- 241000255925 Diptera Species 0.000 description 1
- 208000003556 Dry Eye Syndromes Diseases 0.000 description 1
- 206010013774 Dry eye Diseases 0.000 description 1
- 208000000059 Dyspnea Diseases 0.000 description 1
- 206010013975 Dyspnoeas Diseases 0.000 description 1
- 102100025137 Early activation antigen CD69 Human genes 0.000 description 1
- 206010015150 Erythema Diseases 0.000 description 1
- 206010015943 Eye inflammation Diseases 0.000 description 1
- 206010015958 Eye pain Diseases 0.000 description 1
- 229940124602 FDA-approved drug Drugs 0.000 description 1
- 206010016059 Facial pain Diseases 0.000 description 1
- 206010053172 Fatal outcomes Diseases 0.000 description 1
- 102000008857 Ferritin Human genes 0.000 description 1
- 108050000784 Ferritin Proteins 0.000 description 1
- 238000008416 Ferritin Methods 0.000 description 1
- 206010016654 Fibrosis Diseases 0.000 description 1
- 206010016717 Fistula Diseases 0.000 description 1
- BJGNCJDXODQBOB-UHFFFAOYSA-N Fivefly Luciferin Natural products OC(=O)C1CSC(C=2SC3=CC(O)=CC=C3N=2)=N1 BJGNCJDXODQBOB-UHFFFAOYSA-N 0.000 description 1
- 238000012413 Fluorescence activated cell sorting analysis Methods 0.000 description 1
- 206010017533 Fungal infection Diseases 0.000 description 1
- 206010017577 Gait disturbance Diseases 0.000 description 1
- 206010018364 Glomerulonephritis Diseases 0.000 description 1
- 108010068370 Glutens Proteins 0.000 description 1
- 206010018498 Goitre Diseases 0.000 description 1
- 208000024869 Goodpasture syndrome Diseases 0.000 description 1
- 206010072579 Granulomatosis with polyangiitis Diseases 0.000 description 1
- 208000035895 Guillain-Barré syndrome Diseases 0.000 description 1
- 208000018565 Hemochromatosis Diseases 0.000 description 1
- 102000001554 Hemoglobins Human genes 0.000 description 1
- 108010054147 Hemoglobins Proteins 0.000 description 1
- 208000035186 Hemolytic Autoimmune Anemia Diseases 0.000 description 1
- 241000711549 Hepacivirus C Species 0.000 description 1
- 241000700721 Hepatitis B virus Species 0.000 description 1
- 208000005176 Hepatitis C Diseases 0.000 description 1
- 101000934374 Homo sapiens Early activation antigen CD69 Proteins 0.000 description 1
- 241000341655 Human papillomavirus type 16 Species 0.000 description 1
- 206010020565 Hyperaemia Diseases 0.000 description 1
- 208000008454 Hyperhidrosis Diseases 0.000 description 1
- 206010020772 Hypertension Diseases 0.000 description 1
- 206010020880 Hypertrophy Diseases 0.000 description 1
- 206010061598 Immunodeficiency Diseases 0.000 description 1
- 206010062016 Immunosuppression Diseases 0.000 description 1
- 238000012404 In vitro experiment Methods 0.000 description 1
- 206010021639 Incontinence Diseases 0.000 description 1
- 108010050904 Interferons Proteins 0.000 description 1
- 102000014150 Interferons Human genes 0.000 description 1
- 108010002352 Interleukin-1 Proteins 0.000 description 1
- 102000000589 Interleukin-1 Human genes 0.000 description 1
- 102000051628 Interleukin-1 receptor antagonist Human genes 0.000 description 1
- 108700021006 Interleukin-1 receptor antagonist Proteins 0.000 description 1
- 108010002350 Interleukin-2 Proteins 0.000 description 1
- 208000005615 Interstitial Cystitis Diseases 0.000 description 1
- 208000029523 Interstitial Lung disease Diseases 0.000 description 1
- 206010022941 Iridocyclitis Diseases 0.000 description 1
- 206010022998 Irritability Diseases 0.000 description 1
- 206010023126 Jaundice Diseases 0.000 description 1
- 208000012659 Joint disease Diseases 0.000 description 1
- 206010059176 Juvenile idiopathic arthritis Diseases 0.000 description 1
- 125000002066 L-histidyl group Chemical group [H]N1C([H])=NC(C([H])([H])[C@](C(=O)[*])([H])N([H])[H])=C1[H] 0.000 description 1
- 238000008214 LDL Cholesterol Methods 0.000 description 1
- 108010063045 Lactoferrin Proteins 0.000 description 1
- 102100032241 Lactotransferrin Human genes 0.000 description 1
- 102000001109 Leukocyte L1 Antigen Complex Human genes 0.000 description 1
- 108010069316 Leukocyte L1 Antigen Complex Proteins 0.000 description 1
- NNJVILVZKWQKPM-UHFFFAOYSA-N Lidocaine Chemical compound CCN(CC)CC(=O)NC1=C(C)C=CC=C1C NNJVILVZKWQKPM-UHFFFAOYSA-N 0.000 description 1
- 102000003960 Ligases Human genes 0.000 description 1
- 108090000364 Ligases Proteins 0.000 description 1
- 108060001084 Luciferase Proteins 0.000 description 1
- 239000005089 Luciferase Substances 0.000 description 1
- DDWFXDSYGUXRAY-UHFFFAOYSA-N Luciferin Natural products CCc1c(C)c(CC2NC(=O)C(=C2C=C)C)[nH]c1Cc3[nH]c4C(=C5/NC(CC(=O)O)C(C)C5CC(=O)O)CC(=O)c4c3C DDWFXDSYGUXRAY-UHFFFAOYSA-N 0.000 description 1
- 206010025323 Lymphomas Diseases 0.000 description 1
- 208000030289 Lymphoproliferative disease Diseases 0.000 description 1
- 102000043131 MHC class II family Human genes 0.000 description 1
- 108091054438 MHC class II family Proteins 0.000 description 1
- 241000124008 Mammalia Species 0.000 description 1
- 102000018697 Membrane Proteins Human genes 0.000 description 1
- 108010052285 Membrane Proteins Proteins 0.000 description 1
- 108060004795 Methyltransferase Proteins 0.000 description 1
- 108700011259 MicroRNAs Proteins 0.000 description 1
- 206010049567 Miller Fisher syndrome Diseases 0.000 description 1
- 108020005196 Mitochondrial DNA Proteins 0.000 description 1
- 208000008238 Muscle Spasticity Diseases 0.000 description 1
- 208000010428 Muscle Weakness Diseases 0.000 description 1
- 206010028372 Muscular weakness Diseases 0.000 description 1
- 208000031888 Mycoses Diseases 0.000 description 1
- 102000006386 Myelin Proteins Human genes 0.000 description 1
- 108010083674 Myelin Proteins Proteins 0.000 description 1
- 108091007491 NSP3 Papain-like protease domains Proteins 0.000 description 1
- CMWTZPSULFXXJA-UHFFFAOYSA-N Naproxen Natural products C1=C(C(C)C(O)=O)C=CC2=CC(OC)=CC=C21 CMWTZPSULFXXJA-UHFFFAOYSA-N 0.000 description 1
- 206010029155 Nephropathy toxic Diseases 0.000 description 1
- 206010029164 Nephrotic syndrome Diseases 0.000 description 1
- 208000012902 Nervous system disease Diseases 0.000 description 1
- 206010060860 Neurological symptom Diseases 0.000 description 1
- 108020004711 Nucleic Acid Probes Proteins 0.000 description 1
- 206010061137 Ocular toxicity Diseases 0.000 description 1
- 206010031009 Oral pain Diseases 0.000 description 1
- 206010053159 Organ failure Diseases 0.000 description 1
- 206010068319 Oropharyngeal pain Diseases 0.000 description 1
- 208000001132 Osteoporosis Diseases 0.000 description 1
- 206010033546 Pallor Diseases 0.000 description 1
- 206010033661 Pancytopenia Diseases 0.000 description 1
- 208000031481 Pathologic Constriction Diseases 0.000 description 1
- 208000037273 Pathologic Processes Diseases 0.000 description 1
- 201000011152 Pemphigus Diseases 0.000 description 1
- 241000721454 Pemphigus Species 0.000 description 1
- 206010034960 Photophobia Diseases 0.000 description 1
- ZYFVNVRFVHJEIU-UHFFFAOYSA-N PicoGreen Chemical compound CN(C)CCCN(CCCN(C)C)C1=CC(=CC2=[N+](C3=CC=CC=C3S2)C)C2=CC=CC=C2N1C1=CC=CC=C1 ZYFVNVRFVHJEIU-UHFFFAOYSA-N 0.000 description 1
- 208000002151 Pleural effusion Diseases 0.000 description 1
- 206010035664 Pneumonia Diseases 0.000 description 1
- 238000011529 RT qPCR Methods 0.000 description 1
- 208000035415 Reinfection Diseases 0.000 description 1
- 206010062237 Renal impairment Diseases 0.000 description 1
- 206010061481 Renal injury Diseases 0.000 description 1
- 241000219061 Rheum Species 0.000 description 1
- 208000025747 Rheumatic disease Diseases 0.000 description 1
- 206010039101 Rhinorrhoea Diseases 0.000 description 1
- 206010040021 Sensory abnormalities Diseases 0.000 description 1
- 208000019802 Sexually transmitted disease Diseases 0.000 description 1
- 208000032023 Signs and Symptoms Diseases 0.000 description 1
- 206010040943 Skin Ulcer Diseases 0.000 description 1
- 206010040867 Skin hypertrophy Diseases 0.000 description 1
- 206010041519 Spider naevus Diseases 0.000 description 1
- 208000020339 Spinal injury Diseases 0.000 description 1
- 201000002661 Spondylitis Diseases 0.000 description 1
- 241000191967 Staphylococcus aureus Species 0.000 description 1
- 108010090804 Streptavidin Proteins 0.000 description 1
- 101000874347 Streptococcus agalactiae IgA FC receptor Proteins 0.000 description 1
- 208000006011 Stroke Diseases 0.000 description 1
- 102000004523 Sulfate Adenylyltransferase Human genes 0.000 description 1
- 108010022348 Sulfate adenylyltransferase Proteins 0.000 description 1
- 201000009594 Systemic Scleroderma Diseases 0.000 description 1
- 206010042953 Systemic sclerosis Diseases 0.000 description 1
- 230000006044 T cell activation Effects 0.000 description 1
- 230000024932 T cell mediated immunity Effects 0.000 description 1
- 208000001871 Tachycardia Diseases 0.000 description 1
- QJJXYPPXXYFBGM-LFZNUXCKSA-N Tacrolimus Chemical compound C1C[C@@H](O)[C@H](OC)C[C@@H]1\C=C(/C)[C@@H]1[C@H](C)[C@@H](O)CC(=O)[C@H](CC=C)/C=C(C)/C[C@H](C)C[C@H](OC)[C@H]([C@H](C[C@H]2C)OC)O[C@@]2(O)C(=O)C(=O)N2CCCC[C@H]2C(=O)O1 QJJXYPPXXYFBGM-LFZNUXCKSA-N 0.000 description 1
- AUYYCJSJGJYCDS-LBPRGKRZSA-N Thyrolar Chemical compound IC1=CC(C[C@H](N)C(O)=O)=CC(I)=C1OC1=CC=C(O)C(I)=C1 AUYYCJSJGJYCDS-LBPRGKRZSA-N 0.000 description 1
- 102000011923 Thyrotropin Human genes 0.000 description 1
- 108010061174 Thyrotropin Proteins 0.000 description 1
- 206010044245 Toxic optic neuropathy Diseases 0.000 description 1
- 241000159243 Toxicodendron radicans Species 0.000 description 1
- 241000209140 Triticum Species 0.000 description 1
- 235000021307 Triticum Nutrition 0.000 description 1
- 241000223109 Trypanosoma cruzi Species 0.000 description 1
- 102100040247 Tumor necrosis factor Human genes 0.000 description 1
- 206010067584 Type 1 diabetes mellitus Diseases 0.000 description 1
- 208000025865 Ulcer Diseases 0.000 description 1
- 206010046851 Uveitis Diseases 0.000 description 1
- 102000013127 Vimentin Human genes 0.000 description 1
- 108010065472 Vimentin Proteins 0.000 description 1
- 235000005811 Viola adunca Nutrition 0.000 description 1
- 240000009038 Viola odorata Species 0.000 description 1
- 235000013487 Viola odorata Nutrition 0.000 description 1
- 235000002254 Viola papilionacea Nutrition 0.000 description 1
- 208000021017 Weight Gain Diseases 0.000 description 1
- JLCPHMBAVCMARE-UHFFFAOYSA-N [3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-[[3-[[3-[[3-[[3-[[3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-hydroxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methyl [5-(6-aminopurin-9-yl)-2-(hydroxymethyl)oxolan-3-yl] hydrogen phosphate Polymers Cc1cn(C2CC(OP(O)(=O)OCC3OC(CC3OP(O)(=O)OCC3OC(CC3O)n3cnc4c3nc(N)[nH]c4=O)n3cnc4c3nc(N)[nH]c4=O)C(COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3CO)n3cnc4c(N)ncnc34)n3ccc(N)nc3=O)n3cnc4c(N)ncnc34)n3ccc(N)nc3=O)n3ccc(N)nc3=O)n3ccc(N)nc3=O)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cc(C)c(=O)[nH]c3=O)n3cc(C)c(=O)[nH]c3=O)n3ccc(N)nc3=O)n3cc(C)c(=O)[nH]c3=O)n3cnc4c3nc(N)[nH]c4=O)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)O2)c(=O)[nH]c1=O JLCPHMBAVCMARE-UHFFFAOYSA-N 0.000 description 1
- 206010000059 abdominal discomfort Diseases 0.000 description 1
- 230000003187 abdominal effect Effects 0.000 description 1
- 230000002159 abnormal effect Effects 0.000 description 1
- 230000005856 abnormality Effects 0.000 description 1
- 238000010521 absorption reaction Methods 0.000 description 1
- FHEAIOHRHQGZPC-KIWGSFCNSA-N acetic acid;(2s)-2-amino-3-(4-hydroxyphenyl)propanoic acid;(2s)-2-aminopentanedioic acid;(2s)-2-aminopropanoic acid;(2s)-2,6-diaminohexanoic acid Chemical compound CC(O)=O.C[C@H](N)C(O)=O.NCCCC[C@H](N)C(O)=O.OC(=O)[C@@H](N)CCC(O)=O.OC(=O)[C@@H](N)CC1=CC=C(O)C=C1 FHEAIOHRHQGZPC-KIWGSFCNSA-N 0.000 description 1
- 229940119059 actemra Drugs 0.000 description 1
- 230000004913 activation Effects 0.000 description 1
- 208000024716 acute asthma Diseases 0.000 description 1
- 208000002552 acute disseminated encephalomyelitis Diseases 0.000 description 1
- 208000005652 acute fatty liver of pregnancy Diseases 0.000 description 1
- 208000038016 acute inflammation Diseases 0.000 description 1
- 230000006022 acute inflammation Effects 0.000 description 1
- 238000011374 additional therapy Methods 0.000 description 1
- IRLPACMLTUPBCL-FCIPNVEPSA-N adenosine-5'-phosphosulfate Chemical compound C1=NC=2C(N)=NC=NC=2N1[C@@H]1O[C@@H](CO[P@](O)(=O)OS(O)(=O)=O)[C@H](O)[C@H]1O IRLPACMLTUPBCL-FCIPNVEPSA-N 0.000 description 1
- 150000003838 adenosines Chemical class 0.000 description 1
- 239000002671 adjuvant Substances 0.000 description 1
- 230000002411 adverse Effects 0.000 description 1
- 230000006838 adverse reaction Effects 0.000 description 1
- 239000011543 agarose gel Substances 0.000 description 1
- 238000000246 agarose gel electrophoresis Methods 0.000 description 1
- 238000007844 allele-specific PCR Methods 0.000 description 1
- 230000000961 alloantigen Effects 0.000 description 1
- 102000006707 alpha-beta T-Cell Antigen Receptors Human genes 0.000 description 1
- 108010087408 alpha-beta T-Cell Antigen Receptors Proteins 0.000 description 1
- DKNWSYNQZKUICI-UHFFFAOYSA-N amantadine Chemical compound C1C(C2)CC3CC2CC1(N)C3 DKNWSYNQZKUICI-UHFFFAOYSA-N 0.000 description 1
- 229960003805 amantadine Drugs 0.000 description 1
- 210000004381 amniotic fluid Anatomy 0.000 description 1
- 229960004238 anakinra Drugs 0.000 description 1
- 229940044094 angiotensin-converting-enzyme inhibitor Drugs 0.000 description 1
- 239000005557 antagonist Substances 0.000 description 1
- 201000004612 anterior uveitis Diseases 0.000 description 1
- 239000003242 anti bacterial agent Substances 0.000 description 1
- 230000001760 anti-analgesic effect Effects 0.000 description 1
- 230000001430 anti-depressive effect Effects 0.000 description 1
- 230000003110 anti-inflammatory effect Effects 0.000 description 1
- 229940088710 antibiotic agent Drugs 0.000 description 1
- 239000000935 antidepressant agent Substances 0.000 description 1
- 229940005513 antidepressants Drugs 0.000 description 1
- 210000000612 antigen-presenting cell Anatomy 0.000 description 1
- 230000000890 antigenic effect Effects 0.000 description 1
- 229940125715 antihistaminic agent Drugs 0.000 description 1
- 239000000739 antihistaminic agent Substances 0.000 description 1
- 239000003435 antirheumatic agent Substances 0.000 description 1
- 230000036506 anxiety Effects 0.000 description 1
- 230000036528 appetite Effects 0.000 description 1
- 235000019789 appetite Nutrition 0.000 description 1
- 238000000149 argon plasma sintering Methods 0.000 description 1
- 238000003491 array Methods 0.000 description 1
- 210000001188 articular cartilage Anatomy 0.000 description 1
- 238000007845 assembly PCR Methods 0.000 description 1
- 238000007846 asymmetric PCR Methods 0.000 description 1
- 230000001363 autoimmune Effects 0.000 description 1
- 201000000448 autoimmune hemolytic anemia Diseases 0.000 description 1
- 208000027625 autoimmune inner ear disease Diseases 0.000 description 1
- 201000003710 autoimmune thrombocytopenic purpura Diseases 0.000 description 1
- 229940003504 avonex Drugs 0.000 description 1
- 229960000794 baclofen Drugs 0.000 description 1
- 208000022362 bacterial infectious disease Diseases 0.000 description 1
- 230000004888 barrier function Effects 0.000 description 1
- 208000013404 behavioral symptom Diseases 0.000 description 1
- 229940049706 benzodiazepine Drugs 0.000 description 1
- 150000001557 benzodiazepines Chemical class 0.000 description 1
- 230000002146 bilateral effect Effects 0.000 description 1
- 210000000941 bile Anatomy 0.000 description 1
- 239000012472 biological sample Substances 0.000 description 1
- 229960002685 biotin Drugs 0.000 description 1
- 239000011616 biotin Substances 0.000 description 1
- 230000036772 blood pressure Effects 0.000 description 1
- 210000000476 body water Anatomy 0.000 description 1
- 231100000366 bone marrow toxicity Toxicity 0.000 description 1
- 210000000481 breast Anatomy 0.000 description 1
- 238000010804 cDNA synthesis Methods 0.000 description 1
- 229940046731 calcineurin inhibitors Drugs 0.000 description 1
- 210000000845 cartilage Anatomy 0.000 description 1
- 230000011712 cell development Effects 0.000 description 1
- 239000006285 cell suspension Substances 0.000 description 1
- 238000002659 cell therapy Methods 0.000 description 1
- 239000003795 chemical substances by application Substances 0.000 description 1
- 229940127243 cholinergic drug Drugs 0.000 description 1
- 208000023819 chronic asthma Diseases 0.000 description 1
- 208000025302 chronic primary adrenal insufficiency Diseases 0.000 description 1
- 231100000749 chronicity Toxicity 0.000 description 1
- 238000003776 cleavage reaction Methods 0.000 description 1
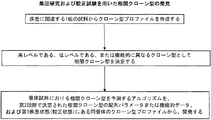
- 238000011509 clonal analysis Methods 0.000 description 1
- 238000010367 cloning Methods 0.000 description 1
- GKTWGGQPFAXNFI-HNNXBMFYSA-N clopidogrel Chemical compound C1([C@H](N2CC=3C=CSC=3CC2)C(=O)OC)=CC=CC=C1Cl GKTWGGQPFAXNFI-HNNXBMFYSA-N 0.000 description 1
- 230000024203 complement activation Effects 0.000 description 1
- 238000012790 confirmation Methods 0.000 description 1
- 208000018631 connective tissue disease Diseases 0.000 description 1
- 238000007596 consolidation process Methods 0.000 description 1
- 208000010247 contact dermatitis Diseases 0.000 description 1
- 230000036461 convulsion Effects 0.000 description 1
- 229940111134 coxibs Drugs 0.000 description 1
- 108010061103 cyclic citrullinated peptide Proteins 0.000 description 1
- 239000003255 cyclooxygenase 2 inhibitor Substances 0.000 description 1
- 238000004163 cytometry Methods 0.000 description 1
- 231100000433 cytotoxic Toxicity 0.000 description 1
- 230000001472 cytotoxic effect Effects 0.000 description 1
- 238000007405 data analysis Methods 0.000 description 1
- 239000000850 decongestant Substances 0.000 description 1
- 229940124581 decongestants Drugs 0.000 description 1
- 230000006735 deficit Effects 0.000 description 1
- 230000003111 delayed effect Effects 0.000 description 1
- 238000004925 denaturation Methods 0.000 description 1
- 230000036425 denaturation Effects 0.000 description 1
- 210000004443 dendritic cell Anatomy 0.000 description 1
- 238000000432 density-gradient centrifugation Methods 0.000 description 1
- 230000001419 dependent effect Effects 0.000 description 1
- 230000008021 deposition Effects 0.000 description 1
- 230000001066 destructive effect Effects 0.000 description 1
- 238000007435 diagnostic evaluation Methods 0.000 description 1
- 238000012631 diagnostic technique Methods 0.000 description 1
- JXSJBGJIGXNWCI-UHFFFAOYSA-N diethyl 2-[(dimethoxyphosphorothioyl)thio]succinate Chemical compound CCOC(=O)CC(SP(=S)(OC)OC)C(=O)OCC JXSJBGJIGXNWCI-UHFFFAOYSA-N 0.000 description 1
- 230000029087 digestion Effects 0.000 description 1
- 239000000539 dimer Substances 0.000 description 1
- 238000002845 discoloration Methods 0.000 description 1
- 239000002934 diuretic Substances 0.000 description 1
- 229940030606 diuretics Drugs 0.000 description 1
- 208000002173 dizziness Diseases 0.000 description 1
- 208000029444 double vision Diseases 0.000 description 1
- 206010013781 dry mouth Diseases 0.000 description 1
- 230000008482 dysregulation Effects 0.000 description 1
- 206010013990 dysuria Diseases 0.000 description 1
- 238000013399 early diagnosis Methods 0.000 description 1
- 235000013399 edible fruits Nutrition 0.000 description 1
- 239000012636 effector Substances 0.000 description 1
- 210000003162 effector t lymphocyte Anatomy 0.000 description 1
- 210000001513 elbow Anatomy 0.000 description 1
- 238000001962 electrophoresis Methods 0.000 description 1
- 229940073621 enbrel Drugs 0.000 description 1
- 230000002255 enzymatic effect Effects 0.000 description 1
- 210000003979 eosinophil Anatomy 0.000 description 1
- 230000003628 erosive effect Effects 0.000 description 1
- 231100000321 erythema Toxicity 0.000 description 1
- 230000000763 evoking effect Effects 0.000 description 1
- 238000013401 experimental design Methods 0.000 description 1
- 210000003722 extracellular fluid Anatomy 0.000 description 1
- 238000000605 extraction Methods 0.000 description 1
- 230000002349 favourable effect Effects 0.000 description 1
- 210000003608 fece Anatomy 0.000 description 1
- 210000003754 fetus Anatomy 0.000 description 1
- 230000004761 fibrosis Effects 0.000 description 1
- 210000001145 finger joint Anatomy 0.000 description 1
- LIYGYAHYXQDGEP-UHFFFAOYSA-N firefly oxyluciferin Natural products Oc1csc(n1)-c1nc2ccc(O)cc2s1 LIYGYAHYXQDGEP-UHFFFAOYSA-N 0.000 description 1
- 230000003890 fistula Effects 0.000 description 1
- 238000000684 flow cytometry Methods 0.000 description 1
- 230000009187 flying Effects 0.000 description 1
- 230000003325 follicular Effects 0.000 description 1
- 210000000285 follicular dendritic cell Anatomy 0.000 description 1
- 238000009472 formulation Methods 0.000 description 1
- 230000005021 gait Effects 0.000 description 1
- 238000002695 general anesthesia Methods 0.000 description 1
- 230000009395 genetic defect Effects 0.000 description 1
- 238000010353 genetic engineering Methods 0.000 description 1
- 229960003776 glatiramer acetate Drugs 0.000 description 1
- 239000003862 glucocorticoid Substances 0.000 description 1
- 235000021312 gluten Nutrition 0.000 description 1
- 150000004676 glycans Chemical class 0.000 description 1
- 201000003872 goiter Diseases 0.000 description 1
- 150000002343 gold Chemical class 0.000 description 1
- 208000024963 hair loss Diseases 0.000 description 1
- 230000003676 hair loss Effects 0.000 description 1
- 210000002478 hand joint Anatomy 0.000 description 1
- 210000003128 head Anatomy 0.000 description 1
- 230000010370 hearing loss Effects 0.000 description 1
- 231100000888 hearing loss Toxicity 0.000 description 1
- 208000016354 hearing loss disease Diseases 0.000 description 1
- 208000019622 heart disease Diseases 0.000 description 1
- 231100000304 hepatotoxicity Toxicity 0.000 description 1
- 239000000833 heterodimer Substances 0.000 description 1
- 238000007849 hot-start PCR Methods 0.000 description 1
- 235000020256 human milk Nutrition 0.000 description 1
- 210000004251 human milk Anatomy 0.000 description 1
- 229940048921 humira Drugs 0.000 description 1
- 230000028996 humoral immune response Effects 0.000 description 1
- 201000001421 hyperglycemia Diseases 0.000 description 1
- 229960001680 ibuprofen Drugs 0.000 description 1
- 238000007654 immersion Methods 0.000 description 1
- 230000006450 immune cell response Effects 0.000 description 1
- 230000007124 immune defense Effects 0.000 description 1
- 230000008629 immune suppression Effects 0.000 description 1
- 230000005847 immunogenicity Effects 0.000 description 1
- 229940072221 immunoglobulins Drugs 0.000 description 1
- 230000002584 immunomodulator Effects 0.000 description 1
- 238000002650 immunosuppressive therapy Methods 0.000 description 1
- 238000007850 in situ PCR Methods 0.000 description 1
- 238000011273 incision biopsy Methods 0.000 description 1
- 229960000905 indomethacin Drugs 0.000 description 1
- 230000006698 induction Effects 0.000 description 1
- 230000001939 inductive effect Effects 0.000 description 1
- 208000000509 infertility Diseases 0.000 description 1
- 230000036512 infertility Effects 0.000 description 1
- 231100000535 infertility Toxicity 0.000 description 1
- 210000004969 inflammatory cell Anatomy 0.000 description 1
- 230000015788 innate immune response Effects 0.000 description 1
- 238000003780 insertion Methods 0.000 description 1
- 230000037431 insertion Effects 0.000 description 1
- 229940047124 interferons Drugs 0.000 description 1
- 208000028774 intestinal disease Diseases 0.000 description 1
- 230000000968 intestinal effect Effects 0.000 description 1
- 230000003834 intracellular effect Effects 0.000 description 1
- 238000012977 invasive surgical procedure Methods 0.000 description 1
- 238000011835 investigation Methods 0.000 description 1
- 150000002500 ions Chemical class 0.000 description 1
- 230000000366 juvenile effect Effects 0.000 description 1
- 201000002215 juvenile rheumatoid arthritis Diseases 0.000 description 1
- 208000017169 kidney disease Diseases 0.000 description 1
- 229940054136 kineret Drugs 0.000 description 1
- 210000003127 knee Anatomy 0.000 description 1
- CSSYQJWUGATIHM-IKGCZBKSSA-N l-phenylalanyl-l-lysyl-l-cysteinyl-l-arginyl-l-arginyl-l-tryptophyl-l-glutaminyl-l-tryptophyl-l-arginyl-l-methionyl-l-lysyl-l-lysyl-l-leucylglycyl-l-alanyl-l-prolyl-l-seryl-l-isoleucyl-l-threonyl-l-cysteinyl-l-valyl-l-arginyl-l-arginyl-l-alanyl-l-phenylal Chemical compound C([C@H](N)C(=O)N[C@@H](CCCCN)C(=O)N[C@@H](CS)C(=O)N[C@@H](CCCNC(N)=N)C(=O)N[C@@H](CCCNC(N)=N)C(=O)N[C@@H](CC=1C2=CC=CC=C2NC=1)C(=O)N[C@@H](CCC(N)=O)C(=O)N[C@@H](CC=1C2=CC=CC=C2NC=1)C(=O)N[C@@H](CCCNC(N)=N)C(=O)N[C@@H](CCSC)C(=O)N[C@@H](CCCCN)C(=O)N[C@@H](CCCCN)C(=O)N[C@@H](CC(C)C)C(=O)NCC(=O)N[C@@H](C)C(=O)N1CCC[C@H]1C(=O)N[C@@H](CO)C(=O)N[C@@H]([C@@H](C)CC)C(=O)N[C@@H]([C@@H](C)O)C(=O)N[C@@H](CS)C(=O)N[C@@H](C(C)C)C(=O)N[C@@H](CCCNC(N)=N)C(=O)N[C@@H](CCCNC(N)=N)C(=O)N[C@@H](C)C(=O)N[C@@H](CC=1C=CC=CC=1)C(O)=O)C1=CC=CC=C1 CSSYQJWUGATIHM-IKGCZBKSSA-N 0.000 description 1
- 229940078795 lactoferrin Drugs 0.000 description 1
- 235000021242 lactoferrin Nutrition 0.000 description 1
- 238000000370 laser capture micro-dissection Methods 0.000 description 1
- 230000002045 lasting effect Effects 0.000 description 1
- 231100000518 lethal Toxicity 0.000 description 1
- 230000001665 lethal effect Effects 0.000 description 1
- 150000002617 leukotrienes Chemical class 0.000 description 1
- 229960004194 lidocaine Drugs 0.000 description 1
- 238000007834 ligase chain reaction Methods 0.000 description 1
- 229940063721 lioresal Drugs 0.000 description 1
- 208000019423 liver disease Diseases 0.000 description 1
- 238000007449 liver function test Methods 0.000 description 1
- 208000018883 loss of balance Diseases 0.000 description 1
- 238000005461 lubrication Methods 0.000 description 1
- 230000001926 lymphatic effect Effects 0.000 description 1
- 238000010801 machine learning Methods 0.000 description 1
- 238000007898 magnetic cell sorting Methods 0.000 description 1
- 239000006249 magnetic particle Substances 0.000 description 1
- 206010025482 malaise Diseases 0.000 description 1
- 210000003794 male germ cell Anatomy 0.000 description 1
- 210000003826 marginal zone b cell Anatomy 0.000 description 1
- 210000001806 memory b lymphocyte Anatomy 0.000 description 1
- 210000003071 memory t lymphocyte Anatomy 0.000 description 1
- 230000002175 menstrual effect Effects 0.000 description 1
- 230000003340 mental effect Effects 0.000 description 1
- 108020004999 messenger RNA Proteins 0.000 description 1
- 229910052751 metal Inorganic materials 0.000 description 1
- 239000002184 metal Substances 0.000 description 1
- 239000002679 microRNA Substances 0.000 description 1
- 230000003278 mimic effect Effects 0.000 description 1
- 229960001156 mitoxantrone Drugs 0.000 description 1
- 230000037230 mobility Effects 0.000 description 1
- 239000003147 molecular marker Substances 0.000 description 1
- 210000001616 monocyte Anatomy 0.000 description 1
- 230000036651 mood Effects 0.000 description 1
- 229940072709 motrin Drugs 0.000 description 1
- 210000003097 mucus Anatomy 0.000 description 1
- 229960003816 muromonab-cd3 Drugs 0.000 description 1
- 210000003205 muscle Anatomy 0.000 description 1
- 208000016334 muscle symptom Diseases 0.000 description 1
- 206010028417 myasthenia gravis Diseases 0.000 description 1
- 229960000951 mycophenolic acid Drugs 0.000 description 1
- HPNSFSBZBAHARI-RUDMXATFSA-N mycophenolic acid Chemical compound OC1=C(C\C=C(/C)CCC(O)=O)C(OC)=C(C)C2=C1C(=O)OC2 HPNSFSBZBAHARI-RUDMXATFSA-N 0.000 description 1
- 210000005012 myelin Anatomy 0.000 description 1
- 210000003007 myelin sheath Anatomy 0.000 description 1
- 229960002009 naproxen Drugs 0.000 description 1
- CMWTZPSULFXXJA-VIFPVBQESA-N naproxen Chemical compound C1=C([C@H](C)C(O)=O)C=CC2=CC(OC)=CC=C21 CMWTZPSULFXXJA-VIFPVBQESA-N 0.000 description 1
- 208000010753 nasal discharge Diseases 0.000 description 1
- 231100000417 nephrotoxicity Toxicity 0.000 description 1
- 230000007694 nephrotoxicity Effects 0.000 description 1
- 210000000653 nervous system Anatomy 0.000 description 1
- 238000007857 nested PCR Methods 0.000 description 1
- 230000004770 neurodegeneration Effects 0.000 description 1
- 238000002610 neuroimaging Methods 0.000 description 1
- 238000010984 neurological examination Methods 0.000 description 1
- 230000007658 neurological function Effects 0.000 description 1
- 230000002232 neuromuscular Effects 0.000 description 1
- 210000002569 neuron Anatomy 0.000 description 1
- 230000007823 neuropathy Effects 0.000 description 1
- 201000001119 neuropathy Diseases 0.000 description 1
- 230000007935 neutral effect Effects 0.000 description 1
- 238000011457 non-pharmacological treatment Methods 0.000 description 1
- 239000002853 nucleic acid probe Substances 0.000 description 1
- 230000005257 nucleotidylation Effects 0.000 description 1
- 238000001584 occupational therapy Methods 0.000 description 1
- 231100000327 ocular toxicity Toxicity 0.000 description 1
- 210000004248 oligodendroglia Anatomy 0.000 description 1
- 229940127240 opiate Drugs 0.000 description 1
- 239000000014 opioid analgesic Substances 0.000 description 1
- 229940005483 opioid analgesics Drugs 0.000 description 1
- 238000011369 optimal treatment Methods 0.000 description 1
- 230000000399 orthopedic effect Effects 0.000 description 1
- JJVOROULKOMTKG-UHFFFAOYSA-N oxidized Photinus luciferin Chemical compound S1C2=CC(O)=CC=C2N=C1C1=NC(=O)CS1 JJVOROULKOMTKG-UHFFFAOYSA-N 0.000 description 1
- 229940094443 oxytocics prostaglandins Drugs 0.000 description 1
- 230000000242 pagocytic effect Effects 0.000 description 1
- 210000000496 pancreas Anatomy 0.000 description 1
- 206010033675 panniculitis Diseases 0.000 description 1
- 208000035824 paresthesia Diseases 0.000 description 1
- 230000009054 pathological process Effects 0.000 description 1
- 230000007170 pathology Effects 0.000 description 1
- 201000001976 pemphigus vulgaris Diseases 0.000 description 1
- 210000003516 pericardium Anatomy 0.000 description 1
- 230000000737 periodic effect Effects 0.000 description 1
- 208000033808 peripheral neuropathy Diseases 0.000 description 1
- 238000001558 permutation test Methods 0.000 description 1
- 229960002895 phenylbutazone Drugs 0.000 description 1
- VYMDGNCVAMGZFE-UHFFFAOYSA-N phenylbutazonum Chemical compound O=C1C(CCCC)C(=O)N(C=2C=CC=CC=2)N1C1=CC=CC=C1 VYMDGNCVAMGZFE-UHFFFAOYSA-N 0.000 description 1
- 238000000554 physical therapy Methods 0.000 description 1
- 239000000902 placebo Substances 0.000 description 1
- 229940068196 placebo Drugs 0.000 description 1
- 238000002616 plasmapheresis Methods 0.000 description 1
- 229940020573 plavix Drugs 0.000 description 1
- 210000004224 pleura Anatomy 0.000 description 1
- 102000054765 polymorphisms of proteins Human genes 0.000 description 1
- 229920001282 polysaccharide Polymers 0.000 description 1
- 239000005017 polysaccharide Substances 0.000 description 1
- 230000004793 poor memory Effects 0.000 description 1
- 231100000857 poor renal function Toxicity 0.000 description 1
- 239000011148 porous material Substances 0.000 description 1
- 230000004481 post-translational protein modification Effects 0.000 description 1
- 230000003389 potentiating effect Effects 0.000 description 1
- 230000002265 prevention Effects 0.000 description 1
- 201000009395 primary hyperaldosteronism Diseases 0.000 description 1
- 238000012545 processing Methods 0.000 description 1
- 230000000750 progressive effect Effects 0.000 description 1
- 150000003180 prostaglandins Chemical class 0.000 description 1
- 230000001681 protective effect Effects 0.000 description 1
- 230000001823 pruritic effect Effects 0.000 description 1
- 208000020016 psychiatric disease Diseases 0.000 description 1
- 230000002685 pulmonary effect Effects 0.000 description 1
- 238000000746 purification Methods 0.000 description 1
- 210000004915 pus Anatomy 0.000 description 1
- 238000001959 radiotherapy Methods 0.000 description 1
- ZAHRKKWIAAJSAO-UHFFFAOYSA-N rapamycin Natural products COCC(O)C(=C/C(C)C(=O)CC(OC(=O)C1CCCCN1C(=O)C(=O)C2(O)OC(CC(OC)C(=CC=CC=CC(C)CC(C)C(=O)C)C)CCC2C)C(C)CC3CCC(O)C(C3)OC)C ZAHRKKWIAAJSAO-UHFFFAOYSA-N 0.000 description 1
- 230000004461 rapid eye movement Effects 0.000 description 1
- 229940038850 rebif Drugs 0.000 description 1
- 210000003289 regulatory T cell Anatomy 0.000 description 1
- 229940116176 remicade Drugs 0.000 description 1
- 210000002345 respiratory system Anatomy 0.000 description 1
- 230000004043 responsiveness Effects 0.000 description 1
- 230000000284 resting effect Effects 0.000 description 1
- 108091008146 restriction endonucleases Proteins 0.000 description 1
- 230000000717 retained effect Effects 0.000 description 1
- 238000003757 reverse transcription PCR Methods 0.000 description 1
- 230000000552 rheumatic effect Effects 0.000 description 1
- 210000003705 ribosome Anatomy 0.000 description 1
- 238000005096 rolling process Methods 0.000 description 1
- 210000004918 root sheath Anatomy 0.000 description 1
- 208000002203 sacroiliac arthritis Diseases 0.000 description 1
- 210000003296 saliva Anatomy 0.000 description 1
- 230000007017 scission Effects 0.000 description 1
- 210000003786 sclera Anatomy 0.000 description 1
- 230000001932 seasonal effect Effects 0.000 description 1
- 210000002374 sebum Anatomy 0.000 description 1
- 230000003248 secreting effect Effects 0.000 description 1
- 210000000582 semen Anatomy 0.000 description 1
- 238000009589 serological test Methods 0.000 description 1
- 206010040560 shock Diseases 0.000 description 1
- 208000013220 shortness of breath Diseases 0.000 description 1
- 238000007860 single-cell PCR Methods 0.000 description 1
- 229960002930 sirolimus Drugs 0.000 description 1
- QFJCIRLUMZQUOT-HPLJOQBZSA-N sirolimus Chemical compound C1C[C@@H](O)[C@H](OC)C[C@@H]1C[C@@H](C)[C@H]1OC(=O)[C@@H]2CCCCN2C(=O)C(=O)[C@](O)(O2)[C@H](C)CC[C@H]2C[C@H](OC)/C(C)=C/C=C/C=C/[C@@H](C)C[C@@H](C)C(=O)[C@H](OC)[C@H](O)/C(C)=C/[C@@H](C)C(=O)C1 QFJCIRLUMZQUOT-HPLJOQBZSA-N 0.000 description 1
- 206010040882 skin lesion Diseases 0.000 description 1
- 231100000444 skin lesion Toxicity 0.000 description 1
- 231100000019 skin ulcer Toxicity 0.000 description 1
- 229940126586 small molecule drug Drugs 0.000 description 1
- SDKPSXWGRWWLKR-UHFFFAOYSA-M sodium;9,10-dioxoanthracene-1-sulfonate Chemical compound [Na+].O=C1C2=CC=CC=C2C(=O)C2=C1C=CC=C2S(=O)(=O)[O-] SDKPSXWGRWWLKR-UHFFFAOYSA-M 0.000 description 1
- 229940087854 solu-medrol Drugs 0.000 description 1
- 238000001179 sorption measurement Methods 0.000 description 1
- 241000894007 species Species 0.000 description 1
- 230000002269 spontaneous effect Effects 0.000 description 1
- 238000010186 staining Methods 0.000 description 1
- 239000007858 starting material Substances 0.000 description 1
- 238000007619 statistical method Methods 0.000 description 1
- 230000036262 stenosis Effects 0.000 description 1
- 208000037804 stenosis Diseases 0.000 description 1
- 230000003637 steroidlike Effects 0.000 description 1
- 230000002739 subcortical effect Effects 0.000 description 1
- 238000007920 subcutaneous administration Methods 0.000 description 1
- 210000004304 subcutaneous tissue Anatomy 0.000 description 1
- 238000006467 substitution reaction Methods 0.000 description 1
- 239000000758 substrate Substances 0.000 description 1
- 230000008093 supporting effect Effects 0.000 description 1
- 238000013268 sustained release Methods 0.000 description 1
- 239000012730 sustained-release form Substances 0.000 description 1
- 230000009747 swallowing Effects 0.000 description 1
- 210000004243 sweat Anatomy 0.000 description 1
- 230000035900 sweating Effects 0.000 description 1
- 230000002194 synthesizing effect Effects 0.000 description 1
- 229940037128 systemic glucocorticoids Drugs 0.000 description 1
- 230000006794 tachycardia Effects 0.000 description 1
- 229960001967 tacrolimus Drugs 0.000 description 1
- QJJXYPPXXYFBGM-SHYZHZOCSA-N tacrolimus Natural products CO[C@H]1C[C@H](CC[C@@H]1O)C=C(C)[C@H]2OC(=O)[C@H]3CCCCN3C(=O)C(=O)[C@@]4(O)O[C@@H]([C@H](C[C@H]4C)OC)[C@@H](C[C@H](C)CC(=C[C@@H](CC=C)C(=O)C[C@H](O)[C@H]2C)C)OC QJJXYPPXXYFBGM-SHYZHZOCSA-N 0.000 description 1
- 210000001138 tear Anatomy 0.000 description 1
- 230000002123 temporal effect Effects 0.000 description 1
- 229960000874 thyrotropin Drugs 0.000 description 1
- 230000001748 thyrotropin Effects 0.000 description 1
- 229940034208 thyroxine Drugs 0.000 description 1
- XUIIKFGFIJCVMT-UHFFFAOYSA-N thyroxine-binding globulin Natural products IC1=CC(CC([NH3+])C([O-])=O)=CC(I)=C1OC1=CC(I)=C(O)C(I)=C1 XUIIKFGFIJCVMT-UHFFFAOYSA-N 0.000 description 1
- 229960000488 tizanidine Drugs 0.000 description 1
- 229960003989 tocilizumab Drugs 0.000 description 1
- 238000003325 tomography Methods 0.000 description 1
- 230000000699 topical effect Effects 0.000 description 1
- 238000007862 touchdown PCR Methods 0.000 description 1
- 231100000331 toxic Toxicity 0.000 description 1
- 230000002588 toxic effect Effects 0.000 description 1
- 230000001988 toxicity Effects 0.000 description 1
- 231100000419 toxicity Toxicity 0.000 description 1
- 238000013518 transcription Methods 0.000 description 1
- 230000035897 transcription Effects 0.000 description 1
- 230000009466 transformation Effects 0.000 description 1
- 230000001131 transforming effect Effects 0.000 description 1
- 230000005945 translocation Effects 0.000 description 1
- 238000011277 treatment modality Methods 0.000 description 1
- YNDXUCZADRHECN-JNQJZLCISA-N triamcinolone acetonide Chemical compound C1CC2=CC(=O)C=C[C@]2(C)[C@]2(F)[C@@H]1[C@@H]1C[C@H]3OC(C)(C)O[C@@]3(C(=O)CO)[C@@]1(C)C[C@@H]2O YNDXUCZADRHECN-JNQJZLCISA-N 0.000 description 1
- 238000009966 trimming Methods 0.000 description 1
- 235000011178 triphosphate Nutrition 0.000 description 1
- 239000001226 triphosphate Substances 0.000 description 1
- 125000002264 triphosphate group Chemical class [H]OP(=O)(O[H])OP(=O)(O[H])OP(=O)(O[H])O* 0.000 description 1
- 201000008827 tuberculosis Diseases 0.000 description 1
- 239000000107 tumor biomarker Substances 0.000 description 1
- 210000004881 tumor cell Anatomy 0.000 description 1
- 239000000439 tumor marker Substances 0.000 description 1
- 230000009959 type I hypersensitivity Effects 0.000 description 1
- 231100000397 ulcer Toxicity 0.000 description 1
- 241001529453 unidentified herpesvirus Species 0.000 description 1
- 210000000689 upper leg Anatomy 0.000 description 1
- 238000010200 validation analysis Methods 0.000 description 1
- 210000005048 vimentin Anatomy 0.000 description 1
- 230000003612 virological effect Effects 0.000 description 1
- XLYOFNOQVPJJNP-UHFFFAOYSA-N water Substances O XLYOFNOQVPJJNP-UHFFFAOYSA-N 0.000 description 1
- 239000002569 water oil cream Substances 0.000 description 1
- 230000003313 weakening effect Effects 0.000 description 1
- 210000004885 white matter Anatomy 0.000 description 1
- 229940000119 zanaflex Drugs 0.000 description 1
Images
Classifications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/10—Processes for the isolation, preparation or purification of DNA or RNA
- C12N15/1034—Isolating an individual clone by screening libraries
- C12N15/1072—Differential gene expression library synthesis, e.g. subtracted libraries, differential screening
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/11—DNA or RNA fragments; Modified forms thereof; Non-coding nucleic acids having a biological activity
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6809—Methods for determination or identification of nucleic acids involving differential detection
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6813—Hybridisation assays
- C12Q1/6827—Hybridisation assays for detection of mutation or polymorphism
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6869—Methods for sequencing
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6876—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6876—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes
- C12Q1/6881—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes for tissue or cell typing, e.g. human leukocyte antigen [HLA] probes
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6876—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes
- C12Q1/6883—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes for diseases caused by alterations of genetic material
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6876—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes
- C12Q1/6883—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes for diseases caused by alterations of genetic material
- C12Q1/6886—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes for diseases caused by alterations of genetic material for cancer
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q2600/00—Oligonucleotides characterized by their use
- C12Q2600/106—Pharmacogenomics, i.e. genetic variability in individual responses to drugs and drug metabolism
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q2600/00—Oligonucleotides characterized by their use
- C12Q2600/118—Prognosis of disease development
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q2600/00—Oligonucleotides characterized by their use
- C12Q2600/156—Polymorphic or mutational markers
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q2600/00—Oligonucleotides characterized by their use
- C12Q2600/158—Expression markers
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q2600/00—Oligonucleotides characterized by their use
- C12Q2600/16—Primer sets for multiplex assays
-
- Y—GENERAL TAGGING OF NEW TECHNOLOGICAL DEVELOPMENTS; GENERAL TAGGING OF CROSS-SECTIONAL TECHNOLOGIES SPANNING OVER SEVERAL SECTIONS OF THE IPC; TECHNICAL SUBJECTS COVERED BY FORMER USPC CROSS-REFERENCE ART COLLECTIONS [XRACs] AND DIGESTS
- Y02—TECHNOLOGIES OR APPLICATIONS FOR MITIGATION OR ADAPTATION AGAINST CLIMATE CHANGE
- Y02A—TECHNOLOGIES FOR ADAPTATION TO CLIMATE CHANGE
- Y02A90/00—Technologies having an indirect contribution to adaptation to climate change
- Y02A90/10—Information and communication technologies [ICT] supporting adaptation to climate change, e.g. for weather forecasting or climate simulation
Description
本出願は2008年11月7日に出願した米国特許出願第61/112,693号の恩典を主張し、これは全体として参照により本明細書に組み入れられる。
免疫系は、先天性免疫系および適応免疫系を含む。先天性免疫系は、外来病原体を認識するために一般的方法を使用する細胞および機構を含む。先天性免疫に関与する細胞には、好中球、ナチュラルキラー細胞、マクロファージ、単球、好塩基球、好酸球、肥満細胞、および樹状細胞が含まれる。これらの細胞は、食作用、および侵入病原体を殺傷する多くの化学物質の放出を行う。加えて、これらの細胞は、補体カスケードおよび炎症を含む先天性免疫防御機構に関与する。最終的に、これらの細胞の一部は、適応免疫系において役割を果たす抗原提示過程に関与する。
[本発明1001]
以下の段階を含む、T細胞および/またはB細胞における組換えDNA配列のプロファイルを決定するための方法:
(a) T細胞および/またはB細胞を含む対象由来の試料を採取する段階;
(b) 該細胞からゲノムDNAの個々の分子を空間的に単離する段階;
(c) ゲノムDNAの空間的に単離された個々の該分子を配列決定する段階;
(d) 該試料からの異なる配列についてそれらのレベルを測定して、組換えDNA配列のプロファイルを作成する段階。
[本発明1002]
以下の段階を含む、T細胞および/またはB細胞における組換えDNA配列のプロファイルを決定するための方法:
(a) T細胞および/またはB細胞を含む対象由来の試料を採取する段階;
(b) 該細胞からゲノムDNAの個々の分子を空間的に単離する段階;
(c) ゲノムDNAの個々の該分子を増幅する段階;
(d) 該増幅DNAを配列決定する段階;ならびに
(e) 該試料からの異なる配列についてそれらのレベルを測定して、組換えDNA配列のプロファイルを作成する段階。
[本発明1003]
以下の段階を含む、T細胞および/またはB細胞における組換えDNA配列のプロファイルを決定するための方法:
(a) T細胞および/またはB細胞を含む対象由来の試料を採取する段階;
(b) 該細胞からゲノムDNAを増幅する段階;
(c) 該増幅DNAの個々の分子を空間的に単離する段階;
(d) 増幅DNAの空間的に単離された個々の該分子を配列決定する段階;ならびに
(e) 該試料からの異なる配列についてそれらのレベルを測定して、組換えDNA配列のプロファイルを作成する段階。
[本発明1004]
以下の段階を含む、T細胞および/またはB細胞における組換えDNA配列のプロファイルを決定するための方法:
(a) T細胞および/またはB細胞を含む対象由来の試料を採取する段階;
(b) 該細胞からゲノムDNAを増幅する段階;
(c) 該増幅DNAの個々の分子を空間的に単離する段階;
(d) 該増幅DNA分子を再増幅する段階;
(e) 該再増幅DNA分子を配列決定する段階;ならびに
(f) 該試料からの異なる配列についてそれらのレベルを測定して、組換えDNA配列のプロファイルを作成する段階。
[本発明1005]
以下の段階を含む、T細胞および/またはB細胞における組換えDNAの配列のプロファイルを決定するための方法:
(a) T細胞および/またはB細胞を含む対象由来の試料を採取する段階;
(b) 該細胞由来のRNAを逆転写してcDNAを形成する段階;
(c) 該cDNAの個々の分子を空間的に単離する段階;
(d) 任意で、cDNAの空間的に単離された個々の該分子を再増幅する段階;
(e) 該cDNAおよび/または再増幅cDNAを配列決定する段階;ならびに
(f) 該試料からの異なる配列についてそれらのレベルを測定して、組換えDNA配列のプロファイルを作成する段階。
[本発明1006]
以下の段階を含む、T細胞および/またはB細胞における組換えDNA配列のプロファイルを決定するための方法:
(a) T細胞および/またはB細胞を含む対象由来の試料を採取する段階;
(b) 該試料中の個々の細胞を空間的に単離する段階;
(c) 該細胞由来の核酸の個々の分子を配列決定する段階;ならびに
(d) 該試料からの異なる配列についてそれらのレベルを測定して、組換えDNA配列のプロファイルを作成する段階。
[本発明1007]
増幅および/または再増幅段階が、PCR、多重PCR、TMA、NASBA、またはLAMPを含む、本発明1001〜1005のいずれかの方法。
[本発明1008]
空間的に単離する段階が、細菌を形質転換するために用いられるベクターに前記DNAもしくはcDNAをサブクローニングすること、固体支持体上で前記DNAもしくはcDNAを二次元に分離すること、ミセルを有する溶液中で前記DNAもしくはcDNAを三次元に分離すること、または微小反応チャンバーを用いて分子を分離することを含む、本発明1001〜1005のいずれかの方法。
[本発明1009]
増幅および/または再増幅段階が、サブクローニングしたDNAもしくはcDNAを保有する細菌の増殖、スライド上でのDNAもしくはcDNAの増幅、またはビーズ上でのDNAもしくはcDNAの増幅によるものである、本発明1001〜1005のいずれかの方法。
[本発明1010]
配列決定段階がジデオキシ配列決定を含む、本発明1001〜1006のいずれかの方法。
[本発明1011]
配列決定段階が、可逆的終結標識ヌクレオチドを用いた合成による配列決定を含む、本発明1001〜1006のいずれかの方法。
[本発明1012]
配列決定段階が、ヌクレオチド取り込み時のピロリン酸放出の検出を含む、本発明1001〜1006のいずれかの方法。
[本発明1013]
配列決定段階が、標識オリゴヌクレオチドプローブのライブラリーへのアレル特異的ハイブリダイゼーションを含む、本発明1001〜1006のいずれかの方法。
[本発明1014]
配列決定段階が、標識オリゴヌクレオチドプローブのライブラリーへのアレル特異的ハイブリダイゼーションとそれに続く該プローブの連結とを用いた合成による配列決定を含む、本発明1001〜1006のいずれかの方法。
[本発明1015]
配列決定段階が、重合工程中の標識ヌクレオチドの取り込みのリアルタイムモニタリングを含む、本発明1001〜1006のいずれかの方法。
[本発明1016]
組換えDNA配列がT細胞受容体遺伝子および/または免疫グロブリン遺伝子を含む、本発明1001〜1006のいずれかの方法。
[本発明1017]
配列決定段階が、免疫グロブリン遺伝子および/またはT細胞受容体遺伝子の完全クローン配列のサブセットを配列決定することを含む、本発明1001〜1006のいずれかの方法。
[本発明1018]
完全クローン配列のサブセットが、免疫グロブリン遺伝子もしくはT細胞受容体遺伝子のV-D結合部、D-J結合部、免疫グロブリン遺伝子もしくはT細胞受容体遺伝子の完全な可変領域、抗原認識領域、または相補性決定領域3(CDR3)を含む、本発明1017の方法。
[本発明1019]
T細胞受容体遺伝子がT細胞受容体β遺伝子を含む、本発明1017の方法。
[本発明1020]
免疫グロブリン遺伝子が免疫グロブリン重鎖遺伝子を含む、本発明1017の方法。
[本発明1021]
増幅または再増幅段階が、Vセグメントと相補的な複数のプライマー、およびCセグメントと相補的な1つのプライマーを含む、本発明1001〜1006のいずれかの方法。
[本発明1022]
増幅または再増幅段階が、Vセグメントと相補的な複数のプライマー、およびCセグメントと相補的な複数のプライマーを含む、本発明1001〜1006のいずれかの方法。
[本発明1023]
Vセグメントと相補的な複数のプライマーが、各Vセグメントに対する少なくとも3種の異なるプライマーを含み、Cセグメントと相補的な複数のプライマーが、少なくとも1種、少なくとも2種、少なくとも3種、少なくとも4種、少なくとも5種、または少なくとも6種のプライマーを含む、本発明1022の方法。
[本発明1024]
T細胞および/またはB細胞が全T細胞および/またはB細胞のサブセットである、本発明1001〜1006のいずれかの方法。
[本発明1025]
T細胞のサブセットがCD4+細胞、CD8+細胞、またはCD27 高 細胞である、本発明1024の方法。
[本発明1026]
試料が、少なくとも100,000個、少なくとも500,000個、少なくとも750,000個、または少なくとも1,000,000個のT細胞を含む、本発明1001〜1006のいずれかの方法。
[本発明1027]
配列決定段階が、1回の実行当たり少なくとも1000件の読み取り、1回の実行当たり少なくとも10,000件の読み取り、1回の実行当たり少なくとも100,000件の読み取り、または1回の実行当たり少なくとも1,000,000件の読み取りを含む、本発明1001〜1006のいずれかの方法。
[本発明1028]
配列決定段階が、1回の読み取り当たり約30 bp、約40 bp、約50 bp、約60 bp、約70 bp、約80 bp、約90 bp、約100 bp、約110 bp、または約120 bpを作成することを含む、本発明1001〜1006のいずれかの方法。
[本発明1029]
対象が自己免疫疾患の再燃(flare)状態にある時点で試料を採取する、本発明1001〜1006のいずれかの方法。
[本発明1030]
全身性エリテマトーデスを有するかまたはそれを有する疑いのある対象から試料を採取する、本発明1001〜1006のいずれかの方法。
[本発明1031]
以下の段階を含む、対象における1つまたは複数の相関クローン型を決定するための方法:
(a) 疾患の第1状態に関連する少なくとも1つの対象由来の試料から空間的に単離された個々の分子を核酸配列決定することにより、1つまたは複数のクローン型プロファイルを作成する段階、および
(b) その1つまたは複数のクローン型プロファイルに基づいて、対象における1つまたは複数の相関クローン型を決定する段階。
[本発明1032]
少なくとも1つの試料が、疾患に罹患した組織に由来する、本発明1031の方法。
[本発明1033]
1つまたは複数の相関クローン型の決定が、少なくとも2つの試料からのクローン型プロファイルを比較することを含む、本発明1031の方法。
[本発明1034]
疾患の第1状態が、疾患のピーク状態である、本発明1031の方法。
[本発明1035]
1つまたは複数の相関クローン型が、疾患のピーク状態において存在する、本発明1034の方法。
[本発明1036]
1つまたは複数の相関クローン型が、疾患のピーク状態において存在しない、本発明1034の方法。
[本発明1037]
1つまたは複数の相関クローン型が、疾患のピーク状態において高い、本発明1034の方法。
[本発明1038]
1つまたは複数の相関クローン型が、疾患のピーク状態において低い、本発明1034の方法。
[本発明1039]
試料がT細胞および/またはB細胞を含む、本発明1031の方法。
[本発明1040]
T細胞および/またはB細胞がT細胞および/またはB細胞のサブセットを含む、本発明1039の方法。
[本発明1041]
T細胞および/またはB細胞のサブセットが、マーカーとの相互作用によって濃縮される、本発明1040の方法。
[本発明1042]
マーカーが、T細胞および/またはB細胞のサブセット上の細胞表面マーカーである、本発明1041の方法。
[本発明1043]
T細胞および/またはB細胞のサブセットが、疾患において特異的に存在する抗原と相互作用する、本発明1039の方法。
[本発明1044]
疾患が全身性エリテマトーデスまたは多発性硬化症である、本発明1031の方法。
[本発明1045]
以下の段階を含む、疾患を有する対象に由来する任意の試料における1つまたは複数の相関クローン型を予測し得るアルゴリズムを開発するための方法:
(a) 疾患に関連する1組の試料から複数のクローン型プロファイルを作成する段階、
(b) その1組の試料から1つまたは複数の相関クローン型を同定する段階、
(c) (b)において同定された1つまたは複数の相関クローン型からの配列パラメータおよび/または機能的データを用いて、疾患を有する対象に由来する任意の試料における相関クローン型を予測し得るアルゴリズムを開発する段階。
[本発明1046]
疾患に罹患した1つまたは複数の組織から1組の試料を採取する、本発明1045の方法。
[本発明1047]
1つまたは複数の相関クローン型の同定が、少なくとも2つの試料からのクローン型プロファイルを比較することを含む、本発明1045の方法。
[本発明1048]
機能的データが、T細胞および/もしくはB細胞表面上のマーカーの結合能、またはT細胞もしくはB細胞による抗原との相互作用を含む、本発明1045の方法。
[本発明1049]
配列パラメータが、核酸配列および予測されるアミノ酸配列を含む、本発明1045の方法。
[本発明1050]
試料が、疾患のピーク状態にある1つまたは複数の個体に由来する、本発明1045の方法。
[本発明1051]
1つまたは複数の相関クローン型が、疾患のピーク状態において存在する、本発明1050の方法。
[本発明1052]
1つまたは複数の相関クローン型が、疾患のピーク状態において高レベルである、本発明1050の方法。
[本発明1053]
1つまたは複数の相関クローン型が、疾患のピーク状態において低レベルである、本発明1050の方法。
[本発明1054]
1つまたは複数の相関クローン型が、疾患のピーク状態において存在しない、本発明1050の方法。
[本発明1055]
疾患が全身性エリテマトーデスまたは多発性硬化症である、本発明1045の方法。
[本発明1056]
以下の段階を含む、個体の1つまたは複数の相関クローン型を発見するための方法:
(a) 個体由来の試料からのクローン型プロファイルを、本発明1045のアルゴリズムに入力する段階、および
(b) アルゴリズムを用いて、個体の1つまたは複数の相関クローン型を決定する段階。
[本発明1057]
疾患のピーク状態において試料を採取する、本発明1056の方法。
[本発明1058]
疾患に罹患した組織から試料を採取する、本発明1056の方法。
[本発明1059]
以下の段階を含む、疾患活動性スコアを算出するアルゴリズムを作成するための方法:
(a) 1組の因子を用いて相関クローン型のレベルを疾患活動性スコアに統合するアルゴリズムを開発する段階、
(b) 疾患活動性スコアを、疾患状態に関する臨床データと比較する段階、および
(c) 臨床データと疾患活動性スコアとの相関を最大化するために因子を最適化する段階。
[本発明1060]
以下の段階を含む、個体の疾患状態をモニターするための方法:
(a) 個体由来の試料からのクローン型プロファイルを決定する段階、
(b) 本発明1059において作成された疾患活動性を算出するアルゴリズムに、(a)からのクローン型プロファイル情報を入力する段階、および
(c) 疾患活動性スコアを算出するアルゴリズムを用いて、個体の疾患状態を予測するスコアを作成する段階。
[本発明1061]
個体における1つまたは複数の相関クローン型を決定する段階、および1つまたは複数の相関クローン型の情報をアルゴリズムに入力する段階をさらに含む、本発明1060の方法。
[本発明1062]
個体における1つまたは複数の相関クローン型を決定する段階が、
(a) 疾患の第1状態に関連する少なくとも1つの対象由来の試料から空間的に単離された個々の分子を核酸配列決定することにより、1つまたは複数のクローン型プロファイルを作成すること、および
(b) その1つまたは複数のクローン型プロファイルに基づいて、対象における1つまたは複数の相関クローン型を決定すること
を含む、本発明1061の方法。
[本発明1063]
個体における1つまたは複数の相関クローン型を決定する段階が、
(a) (i) 疾患に関連する1組の試料から複数のクローン型プロファイルを作成する段階と、
(ii) その1組の試料から1つまたは複数の相関クローン型を同定する段階と、
(iii) (ii)において同定された1つまたは複数の相関クローン型からの配列パラメータおよび/または機能的データを用いて、疾患を有する対象に由来する任意の試料における相関クローン型を予測し得るアルゴリズムを開発する段階と
によって開発された、1つまたは複数のクローン型を予測し得るアルゴリズムに、個体由来の試料からのクローン型プロファイルを入力すること、ならびに
(b) 1つまたは複数のクローン型を予測し得るアルゴリズムを用いて、個体の1つまたは複数の相関クローン型を決定すること
を含む、本発明1061の方法。
[本発明1064]
疾患が全身性エリテマトーデスまたは多発性硬化症である、本発明1061の方法。
本明細書において引用した出版物、特許、および特許出願はすべて、個々の出版物、特許、また特許出願が詳細にかつ個別に参照により組み入れられることが示されるのと同程度に、参照により本明細書に組み入れられる。
概要
概して、提供する本発明は、免疫系をプロファイルするために適応免疫細胞のレパートリーをモニターするという課題に、核酸配列決定技法を適用する方法を含む。作成された免疫系のプロファイルは、疾患および障害の診断、ならびに疾患および障害の状態の診断に用いることができる。提供する本発明の免疫プロファイリングの方法は、疾患および障害をモニターするのに、ならびに疾患および障害の治療を評価するのに用いることができる。提供する本発明の方法を適用することができるこれらの疾患および障害には、全身性エリテマトーデス(SLE)、多発性硬化症(MS)、関節リウマチ(RA)、および強直性脊椎炎を含む自己免疫疾患が含まれる。提供する本発明の方法は、移植片拒絶反応および免疫老化の診断、モニタリング、および治療に適用することができる。さらに、提供する本発明の免疫プロファイリングの方法は、癌および感染症を含む、免疫系に関連するその他の疾患を診断する、モニターする、および治療するのに用いることができる。
A. 概要
提供する本発明の方法を用いて、対象由来の試料における組換えDNA配列またはクローン型のプロファイルを作成することができる。
1. 対象
提供する本発明の方法は、対象または個体(例えば、患者)由来の試料を使用することができる。対象は、例えば自己免疫疾患患者などの患者であってよい。対象は、感染症患者または癌患者であってよい。対象は、例えばヒトなどの哺乳動物であってよい。対象は男性または女性であってよい。対象は、乳児、小児、または成人であってよい。
提供する本発明の方法において用いられる試料には、例えば、胎児を取り囲む羊水、房水、胆汁、血液および血漿、耳垢(cerumen)(耳垢(earwax))、カウパー液または射精前液、乳糜、糜粥、腟液(female ejaculate)、間質液、リンパ液、月経血、母乳、粘液(鼻汁および痰を含む)、胸水、膿汁、唾液、皮脂(sebum)(皮脂(skin oil))、精液、血清、汗、涙、尿、腟液(vaginal lubrication)、嘔吐物、分泌液(water)、糞便を含む対象由来の体液、脳および脊髄を取り囲む脳脊髄液、骨関節を取り囲む滑液、細胞内の液体である細胞内液、および眼球内の液体である硝子体液を含む体内液が含まれ得る。1つの態様において、試料は血液試料である。血液試料は、約0.1、0.2、0.3、0.4、0.5、0.6、0.7、0.8、0.9、1.0、1.5、2.0、2.5、3.0、3.5、4.0、4.5、または5.0 mLであってよい。対象が多発性硬化症を有する場合、試料は脳脊髄液(CSF)であってよく、対象が関節リウマチを有する場合、試料は滑液であってよく、および対象が全身性ループスを有する場合、試料は皮膚(またはその他の器官)生検標本であってよい。1つの態様では、病状を反映する可能性が最も高い利用可能な体液/組織からクローン型を同定し、その後、例えば血液のような別の体液から該クローン型のレベルをモニターすることができる。
1. TCR遺伝子およびBCR遺伝子の特徴
それぞれ個々の適応免疫細胞のDNAおよびそれらの関連RNA転写産物中に特定できる組換えが存在するため、提供する本発明の方法においてRNAまたはDNAのいずれかを配列決定することができる。T細胞またはB細胞由来の組換え配列は、クローン型とも称され得る。DNAまたはRNAは、T細胞受容体(TCR)遺伝子、または抗体をコードする免疫グロブリン(Ig)遺伝子の配列に相当し得る。例えば、DNAおよびRNAは、TCRのα、β、γ、またはδ鎖をコードする配列に相当し得る。大多数のT細胞において、TCRはα鎖およびβ鎖からなるヘテロ二量体である。TCRα鎖はVJ組換えによって生成され、β鎖受容体はV(D)J組換えによって生成される。TCRβ鎖に関して、ヒトではVセグメント48個、Dセグメント2個、およびJセグメント13個が存在する。2つの結合部のそれぞれにおいて、いくつかの塩基が欠失され、また他の塩基が付加され得る(NヌクレオチドおよびPヌクレオチドと称される)。少数のT細胞では、TCRはγ鎖およびδデルタ鎖からなる。TCRγ鎖はVJ組換えによって生成され、TCRδ鎖はV(D)J組換えによって生成される(Kenneth Murphy, Paul Travers, and Mark Walport, Janeway's Immunology 7th edition, Garland Science, 2007、全体として参照により本明細書に組み入れられる)。
ポリメラーゼ連鎖反応(PCR)を用いて、細胞の収集物から関連領域を増幅することができる。転写媒介増幅法(TMA)を用いて、標的核酸からRNA単位複製配列を生成することができる。細胞はそれぞれ独自の特徴を保有するため、各細胞に由来する核酸を個別に解析することができる。
プールから核酸を単離する方法には、核酸をDNAベクターにサブクローニングし、細菌を形質転換すること(細菌クローニング)、固体基質(例えば、スライドガラス)上での二次元での分子の空間的分離、ミセルを有する溶液中での三次元での核酸の空間的分離(例えば、ビーズなどの固体表面上に分子を固定化するかまたは固定化せずに、油エマルジョンを用いて達成され得る)、または例えばマイクロ流体もしくはナノ流体チップといった微小反応チャンバーを用いることが含まれる。所与の容積、空間領域、ビーズ、または反応チャンバー中に平均して単一の分子が存在することを確実にするために、希釈を用いることができる。
提供する本発明の方法において、当業者に公知である、核酸を配列決定するための任意の技法を用いることができる。DNA配列決定技法には、標識ターミネーターまたはプライマーおよび平板またはキャピラリーでのゲル分離を用いた古典的ジデオキシ配列決定反応(サンガー法)、可逆的終結標識ヌクレオチドを用いた合成による配列決定、ピロシーケンシング、454配列決定、標識オリゴヌクレオチドプローブのライブラリーへのアレル特異的ハイブリダイゼーション、標識クローンのライブラリーへのアレル特異的ハイブリダイゼーションとそれに続く連結とを用いた合成による配列決定、重合工程中の標識ヌクレオチドの取り込みのリアルタイムモニタリング、ポロニー配列決定、およびSOLiD配列決定が含まれる。分離された分子の配列決定は、ポリメラーゼもしくはリガーゼを用いた連続的なまたは単一の伸長反応によって、およびプローブのライブラリーとの単一のまたは連続的な差次的ハイブリダイゼーションによって、ごく最近実証された。これらの反応は、1億を超える配列を並行して行う最新の商業的応用における実証を含め、多くのクローン配列において並行して行われた。したがって、これらの配列決定アプローチを、T細胞受容体(TCR)および/またはB細胞受容体(BCR)のレパートリーを調べるために用いることができる。
提供する本発明の方法において用いられ得る配列決定技法には、例えば、Helicos True Single Molecule配列決定(tSMS)(Harris T.D. et al. (2008) Science 320:106-109)が含まれる。tSMS技法では、DNA試料をおよそ100〜200ヌクレオチドの鎖に切断し、各DNA鎖の3'末端にポリA配列を付加する。蛍光標識アデノシンヌクレオチドの付加により、各鎖を標識する。次に、フローセル表面に固定化された何百万ものオリゴT捕捉部位を含むフローセルに対して、このDNA鎖をハイブリダイズさせる。鋳型は、鋳型約1億個/cm2の密度であってよい。次にフローセルを例えばHeliScope(商標)シーケンサーなどの装置に取り込むと、レーザーがフローセルの表面を照射し、各鋳型の位置が明らかになる。CCDカメラが、フローセル表面上の鋳型の位置を位置づけ得る。次に鋳型の蛍光標識を切断し、洗浄除去する。DNAポリメラーゼおよび蛍光標識ヌクレオチドを導入することにより、配列決定反応が開始する。オリゴT核酸はプライマーとして働く。ポリメラーゼは、鋳型の指示する様式でプライマーに標識ヌクレオチドを取り込む。ポリメラーゼおよび取り込まれなかったヌクレオチドを除去する。フローセル表面を画像化することにより、蛍光標識ヌクレオチドの取り込みを指示した鋳型を検出する。画像化した後、切断段階により蛍光標識を除去し、所望の読み取り長が達成されるまで、他の蛍光標識ヌクレオチドを用いてこの過程を繰り返す。各ヌクレオチド付加段階と共に配列情報を回収する。
提供する本発明の方法において用いられ得るDNA配列決定技法の別の例は、454配列決定(Roche)(Margulies, M et al. 2005, Nature, 437, 376-380)である。454配列決定は2段階を含む。第1段階では、DNAをおよそ300〜800塩基対の断片に剪断し、断片を平滑末端化する。次に、断片の末端にオリゴヌクレオチドアダプターを連結させる。アダプターは、断片の増幅および配列決定用のプライマーとして働く。例えば5'-ビオチンタグを含むアダプターBを用いて、DNA捕捉ビーズ、例えばストレプトアビジンコーティングビーズに断片を付着させることができる。ビーズに付着している断片を、油-水エマルジョンの液滴内でPCR増幅する。結果は、各ビーズ上のクローン増幅されたDNA断片の複数コピーである。第2段階では、このビーズをウェル(ピコリットルサイズ)中に捕捉する。各DNA断片においてピロシーケンシングを並行して行う。1つまたは複数のヌクレオチドを添加すると光シグナルが生じ、これを配列決定装置においてCCDカメラで記録する。シグナル強度は、取り込まれたヌクレオチドの数に比例する。
提供する本発明の方法において用いられ得るDNA配列決定技法の別の例は、SOLiD技術(Applied Biosystems)である。SOLiD配列決定では、ゲノムDNAを断片に剪断し、断片の5'および3'末端にアダプターを付着させて、断片ライブラリーを作製する。あるいは、断片の5'および3'末端にアダプターを連結し、断片を環状化し、環状化断片を消化して内部アダプターを生成し、得られた断片の5'および3'末端にアダプターを付着させてメイトペアライブラリーを生成することによって、内部アダプターを導入することができる。次に、ビーズ、プライマー、鋳型、およびPCR成分を含むマイクロリアクター中で、クローンビーズ集団を調製する。PCR後、鋳型を変性させ、伸長した鋳型を伴うビーズを分離するようビーズを濃縮する。選択されたビーズ上の鋳型を、スライドガラスへの結合を可能にする3'修飾に供する。
提供する本発明の方法において用いられ得る配列決定技法の別の例は、SOLEXA技術(Illumina)である。SOLEXA配列決定は、折りたたみPCRおよびアンカープライマーを用いた固体表面上でのDNAの増幅に基づいている。ゲノムDNAを断片化し、断片の5'および3'末端にアダプターを付加する。フローセルチャネルの表面に付着しているDNA断片を伸長させ、架橋増幅する。断片は二本鎖になり、この二本鎖分子を変性させる。固相増幅およびそれに続く変性を複数サイクル行うことで、フローセルの各チャネルにおける、同じ鋳型のおよそ1,000コピーの一本鎖DNA分子のクラスターが数百万個生成され得る。プライマー、DNAポリメラーゼ、および4種のフルオロフォア標識された可逆的終結ヌクレオチドを用いて、連続的配列決定を行う。ヌクレオチドの取り込み後、レーザーを用いてフルオロフォアを励起させ、画像を取り込み、第1塩基の独自性を記録する。それぞれ取り込まれた塩基から3'ターミネーターおよびフルオロフォアを除去し、取り込み、検出、および同定段階を繰り返す。
提供する本発明の方法において用いられ得る配列決定技法の別の例には、Pacific Biosciencesの1分子リアルタイム(SMRT(商標))技術が含まれる。SMRTでは、4種のDNA塩基はそれぞれ4種の異なる蛍光色素の1つに付着している。これらの色素はホスホ結合している。単一のDNAポリメラーゼを1分子の鋳型一本鎖DNAと共に、ゼロモード導波路(ZMW)の底に固定化する。ZMWとは、(マイクロ秒で)ZMWの外側に迅速に拡散する蛍光ヌクレオチドのバックグラウンドに対して、DNAポリメラーゼによる単一ヌクレオチドの取り込みの観察を可能にする限局構造である。ヌクレオチドを伸長鎖に取り込むには、数ミリ秒を要する。この間に、蛍光標識が励起され、蛍光シグナルを生成し、蛍光タグが切断される。色素に対応する蛍光の検出により、どの塩基が取り込まれたが示される。この過程を繰り返す。
提供する本発明の方法において用いられ得る配列決定技法の別の例は、ナノポア配列決定(Soni GV and Meller A. (2007) Clin Chem 53: 1996-2001)である。ナノポアとは、直径1ナノメートル程度の細孔である。伝導性流体中でのナノポアの浸漬、およびそれを介した電位の印加により、ナノポアを通したイオンの伝導に起因してわずかな電流が生じる。流れる電流の量は、ナノポアのサイズに感受性がある。DNA分子がナノポアを通過する際、DNA分子上の各ヌクレオチドは異なる程度にナノポアを塞ぐ。したがって、DNA分子がナノポアを通過する際にナノポアを通過する電流の変化は、DNA配列の読み取りを表す。
提供する本発明の方法において用いられ得る配列決定技法の別の例は、(例えば、米国特許出願公開第20090026082号に記載されているように)DNAを配列決定するために化学感受性電界効果トランジスタ(chemFET)アレイを使用することを含む。この技法の一例では、DNA分子を反応チャンバーに入れることができ、ポリメラーゼに結合している配列決定プライマーに鋳型分子をハイブリダイズさせることができる。配列決定プライマーの3'末端における新たな核酸鎖への1つまたは複数の三リン酸の取り込みを、chemFETによって電流の変化により検出することができる。アレイは複数のchemFETセンサーを有し得る。別の例では、単一の核酸をビーズに付着させることができ、ビーズ上で核酸を増幅することができ、各チャンバーがchemFETセンサーを有しているchemFETアレイ上の個々の反応チャンバーに個々のビーズを移すことができ、核酸を配列決定することができる。
提供する本発明の方法において用いられ得る配列決定技法の別の例は、電子顕微鏡を使用することを含む(Moudrianakis E.N. and Beer M. Proc Natl Acad Sci U S A. 1965 Mar;53:564-71)。この技法の一例では、電子顕微鏡を用いて識別可能な金属標識を使用して、個々のDNA分子を標識する。次に、これらの分子を平面上に広げ、電子顕微鏡を用いて画像化して配列を測定する。
単一分子から生じるか、または単一分子由来の増幅物から生じる配列を読むことができる。固体表面上で、または水/油エマルジョン内の微小な区画内で、何百万という単一分子の独立した増幅を並行して行うことができる。各区画内に1分子が入るように、配列決定すべきDNA試料を十分に希釈する、および/または分散させることができる。この希釈に続いてDNA増幅を行って、元のDNA配列のコピーを作製し、すべて同じ配列を有する分子の「クラスター」を生成することができる。次に、これらのクラスターを配列決定することができる。1回の実行で、何百万もの読み取りが作成され得る。増幅配列の所与の鎖の5'末端から開始する配列が作成され得る、および/または相補的配列の5'末端から開始する配列が作成され得る。好ましい態様では、両鎖から配列が作成される、すなわち対をなす末端読み取り(paired end read)が作成される。
A. 相関クローン型 対 非相関クローン型
T細胞およびB細胞受容体配列の膨大なレパートリーのために、特定のヒト健康転帰と相関する個々の細胞を見出す上で課題が生じる。多くの場合、関心対象となるクローン型の配列は、調べる個体に特有である。本発明の方法は、a) 相関クローン型(そのレベルが疾患と相関するクローン型であってよい)とb) 非相関クローン型(そのレベルが疾患と相関しないクローン型であってよい)を識別するための手段を提供する。1つの態様において、相関クローン型は、疾患と正または負の相関のいずれかを示し得る。別の態様において、疾患のピーク状態において存在するが、疾患の非ピーク状態では存在しないクローン型は、相関クローン型であり得る(疾患と正の相関)。別の態様において、疾患の非ピーク状態よりも疾患のピーク状態(または段階)においてより豊富な(すなわち、より高レベルの分子で存在する)クローン型は、相関クローン型であり得る(疾患と正の相関)。別の態様において、疾患のピーク状態において存在しないが、疾患の非ピーク中に存在するクローン型は、相関クローン型であり得る(疾患と負の相関)。別の態様において、疾患の非ピーク状態よりもピーク状態においてより少ないクローン型は、相関クローン型であり得る(疾患と負の相関)。別の態様において、個体の相関クローン型はアルゴリズムによって決定される。
本発明のこの態様では、疾患状態と関連性があるいくつかの試料中に存在するクローン型を調べることによって、相関クローン型を同定する(例えば、図14を参照されたい)。この状態は、疾患のピーク状態にある試料由来の血液(例えば、急性再燃中のMSまたはループス患者由来の血液試料)、またはその個体の疾患に関与するT細胞およびB細胞が濃縮されたと推測される罹患組織であってよい。これらの組織の例は、腎臓炎症を有するループス患者の腎臓生検標本、再燃中のMS患者におけるCSF、関節リウマチ患者の滑液、または癌患者由来の腫瘍試料であってよい。これらの例のすべてにおいて、組織は、(必ずしも原因因子であるわけではないが)疾患に関連する関連T細胞およびB細胞を含む可能性が高い。この方法を用いて疾患に関連するクローン型を同定する場合、クローン型が、その試料中にそれらが検出された個体にのみ関連することは、特筆すべきことである。結果として、疾患を有する任意の所与の個体において相関クローン型を同定するのにこの方法を用いるためには、特定の較正試験が必要となる。
1つの態様において、集団研究を用いて相関クローン型を同定する方法を提供する(例えば、図15を参照されたい)。集団研究の有用性は、疾患状態転帰が判明している個体において確認された相関クローン型に関する特異的情報を一般化して、較正試験を行う必要なしに、そのような相関クローン型が将来の対象すべてにおいて同定され得るようにすることを可能にする点である。特定の1組の相関クローン型の知識を用いて、将来の対象において相関するであろうクローン型の適した特質(パラメータ)に関する規則を抽出することができる。
本発明の1つの態様では、較正試験と集団研究を併用することによって、相関クローン型を同定する(例えば、図17を参照されたい)。本態様では、集団研究は、任意の試料におけるクローン型の予測を可能にするアルゴリズムをもたらすのではなく、集団研究によって、特定の較正クローン型プロファイルが作成された対象に由来する任意の試料における相関クローン型を予測するためのアルゴリズムの開発が可能になる(例えば、図16を参照されたい)。この例は、アルゴリズムを較正するために用いられた臨床的再燃状態中の血液検査を最初に受けた後の疾患の任意の段階における血液試料から測定されたクローン型プロファイルに基づいて、ループス患者における相関クローン型を予測するアルゴリズムの開発であってよい。
集団研究を行うために、訓練セットを用いて、相関クローン型と相関しないクローン型を識別し得る様々なパラメータを試験することにより、相関クローン型の特徴を理解することができる。これらのパラメータには、用いられる配列または特異的なV、D、およびJセグメントが含まれる。1つの態様では、特定の疾患のクローン型が関連エピトープを認識する可能性が高く、よって配列類似性を有し得る場合のように、特異的なVセグメントがいくつかの疾患と相関する可能性がより高いことが示される。さらなる態様に含まれる他のパラメータには、同定される体細胞超突然変異の程度、ならびに症状発現のピーク時におけるクローン型のレベルおよび疾患が比較的非活動性である場合のそのレベルが含まれる。相関クローン型を予測し得る他のパラメータには、非限定的に、1) VまたはJ領域、組み合わせVJ、DJ領域内の短い配列を含む配列モチーフ;2) クローン型の配列長;3) 絶対レベル(分子100万個当たりのクローン数)または順位レベルを含むクローン型のレベル;4) 他のクローン型とのアミノ酸および核酸配列類似性:サイレント変化を有するもの(同じアミノ酸をコードするヌクレオチドの違い)または保存的アミノ酸変化を有するものを含む、他の高度に関連したクローン型の頻度;5) BCRに関して、クローン型における体細胞突然変異のレベル、および/またはいくつかの生殖系列クローン型と体細胞突然変異によって異なる別個のクローン型の数;6) その関連タンパク質が類似の3次元構造を有するクローン型が含まれる。
さらなる態様は、相関クローン型の同定を支援するために機能的データを使用する。例えば、相関クローン型を含む細胞において濃縮されるある種のマーカーを含むT細胞および/またはB細胞を、FACSまたはMACSのような標準的な方法を通じて捕捉することができる。別の態様において、マーカーは細胞表面マーカーである。別の態様において、病理に関連する抗原または罹患組織に対するT細胞および/またはB細胞反応性は、クローン型の病理学的関連性の優れた証拠である。
アルゴリズムを用いて、Immune Loadを計算することができる(例えば、図18を参照されたい)。Immune Loadを用いて、臨床決定を下すことができる。実験(例えば、疾患の第1状態にある対象に由来する試料、および疾患の第2状態にある対象に由来する試料を含む実験)からのデータを用いて、相関および非相関クローン型のレベルに関する情報を単一のスコア(Immune Load)に統合するアルゴリズムを開発することができる。次に、Immune Loadと臨床データとの相関を最大化するために、このアルゴリズムのパラメータを調整することができる。例えば、臨床データは、疾患重症度の臨床的尺度(例えば、多発性硬化症患者に関するMRIにおける病変の程度)であってよい。
1. 較正試験なしでの疾患のモニタリング
本発明の1つの態様では、集団研究を用いて、クローン型およびImmune Loadアルゴリズムを決定する(例えば、図19を参照されたい)。最初に個々の患者を較正する必要なしに、Immune Loadを直接用いることができる。患者が任意の疾患状態にある場合に、この試験を行うことができる。この試験を用いて、上記で開発したアルゴリズムに基づいて、特異的な相関および非相関クローン型を作成することができる。次に、集団研究において作成された第2のアルゴリズムを用いて、Immune Loadを算出することができる。次に、このスコアを臨床的に用いることができる。
提供する本発明の1つの態様では、較正試験、または較正試験および集団研究を用いて、クローン型およびImmune Loadアルゴリズムを決定する(例えば、図20を参照されたい)。最初に較正試験を行うことによって、診療所においてImmune Loadを用いることができる。患者が、Immune Loadアルゴリズムにおいて用いられる相関および非相関クローン型を作成した研究において用いられた第1状態と類似した状態にある場合に、この試験を行うことができる。例えば、自己免疫疾患の再燃状態が、Immune Loadアルゴリズムが導き出された方法であるならば、この状態はそれであってよい。次に、この較正試験を用いて、その後の疾患モニタリング試験において用いるべき特異的な相関および非相関クローン型を作成することができる。この患者の治療における後の時点で、患者に対して別の試験を行い、発見研究において作成されたアルゴリズム、およびこの患者の特異的較正試験において作成されたクローン型レベルのリストを用いて、Immune Loadを算出することができる。次に、このImmune Loadスコアを臨床的に用いることができる。
同じImmune Loadでも、異なる患者に対しては異なることを意味し得る。一例としては、患者の完全な臨床像を考慮する必要がある。試験の観点から、臨床決定を下す際には、Immune Loadのレベルに加えて、速度(経時的なImmune Loadの変化率)および加速(経時的な速度の変化率)を考慮する場合がある。例えば、AutoImm Loadスコアが増加している場合(高速度)、これは自己免疫疾患における初期の再燃を予測し得る。
免疫系はヒトの健康にとって非常に重要であるため、免疫応答を測定する能力は医学において広い応用性がある。本発明は、基礎疾患状態が免疫系によって媒介される場合に、これを理解するために免疫系を使用する能力を教示する。これによって、免疫プロファイルを使用する非常に強力な一連の診断的および予後診断的適用は、多種多様な臨床転帰のリスクを伝え、医師をより効率的に介入させることが可能になる。
対象における自己免疫疾患を診断および治療するために、提供する本発明の方法を用いることができる。自己免疫疾患は、通常の過程を回避して、自己免疫を付与し、身体の組織上の何らかの標的を攻撃する適応免疫細胞を含む。自己免疫疾患には、例えば、急性散在性脳脊髄炎、アジソン病、強直性脊椎炎、抗リン脂質抗体症候群、自己免疫性溶血性貧血、自己免疫性肝炎、自己免疫性内耳疾患、ベーチェット病、水疱性類天疱瘡、セリアック病、シャーガス病、慢性閉塞性肺疾患、皮膚筋炎、1型糖尿病、グッドパスチャー症候群、グレーブス病、ギラン・バレー症候群、橋本甲状腺炎、化膿性汗腺炎、特発性血小板減少性紫斑病、間質性膀胱炎、多発性硬化症、重症筋無力症、神経性筋強直症、尋常性天疱瘡、悪性貧血、多発性筋炎、原発性胆汁性肝硬変、関節リウマチ、強皮症、全身性エリテマトーデス、シェーグレン症候群、および血管炎症候群が含まれる。これらの自己免疫疾患の段階は、提供する本発明の方法を用いて診断することができる。自己免疫疾患の段階に基づいて、対象に治療を示唆することができる。
全身性エリテマトーデス(SLEまたはループス)の状態または段階を決定するために、提供する本発明の方法を用いることができる。SLEは、若年成人(主に女性)が罹患することの多い重篤な自己免疫病態である。これは、皮膚、関節、腎臓、肺、心臓、および中枢神経系を含む多くの器官を侵し、頻繁に障害および場合によっては死を引き起こし得る炎症過程によって特徴づけられる。本疾患は、再燃期およびそれに続く寛解の休止期を特徴とする、非常に予測不可能な経過をたどる。それにもかかわらず、SLEと診断された患者はリウマチ専門医による診察を定期的に受け、様々な深刻な薬物による治療を受ける。これらの薬物には、プレドニゾンなどのステロイド剤、およびCellcept(ミコフェノール酸モフェチル)などの他の免疫抑制剤が含まれる。これらの薬物は器官の損傷を軽減し得るものの、それらは感染症および不妊のリスクを含む重大な副作用を含む。症状のいくつか(例えば、疼痛および疲労)に関して信頼性がないこと、および疾患経過が予測できないことから、薬物用量を目的に合わせることは難しく、結果として一部の患者には過剰治療を招き、他の患者には過少治療を招くことになる。結果として、SLEの治療は、臨床医に重要な臨床的課題をもたらす。
提供する本発明の方法はまた、多発性硬化症(MS)の状態または段階を決定するために用いることもできる。MSは、脳および脊髄(中枢神経系)を侵す疾患である。それぞれの発作の部位および重症度が異なり得るため、症状は様々である。症状発現は数日間、数週間、または数カ月間持続し得る。これらの症状発現は、症状が軽減されるかまたは現れない(寛解)期間と交互に起こる。この疾患は再発する(return)(再発する(relapse))のが一般的である。しかしながら、疾患は寛解期なしに悪化し続ける場合もある。
関節リウマチ患者の疾患状態を測定するために、本方法を用いることができる。関節リウマチ(RA)は、多くの組織および器官を侵し得るが主に関節を攻撃して、関節軟骨の破壊および関節の強直へと進行する場合の多い炎症性滑膜炎を引き起こす慢性全身性炎症障害である。関節リウマチはまた、肺、心膜、胸膜、および強膜における広汎性炎症、ならびにまた最も一般的には皮下の皮下組織における結節性病変を生じ得る。関節リウマチの原因は不明であるが、自己免疫がその慢性化および進行において重要な役割を果たす。
強直性脊椎炎の疾患活動性を検出するために、本方法を用いることができる。強直性脊椎炎(AS、ギリシャ語からankylos、曲がった;spondylos、脊椎)は、以前は脊椎関節炎の一形態であるベヒテレフ病、ベヒテレフ症候群、およびマリー・シュトリュンペル病として知られていたもので、慢性炎症性関節炎でありかつ自己免疫疾患である。これは主に脊椎の関節および骨盤の仙腸関節を侵し、脊椎の最終的な融合を引き起こす。これは、強い遺伝的素因を伴う脊椎関節症の群の1メンバーである。完全な融合により、竹様脊椎として知られる状態である、脊椎の完全な強直が生じる。
癌のリスクを測定するために、これらの方法を用いることができる。癌は先進工業国における死亡原因の第1位になった。したがって、癌の治療方法は必要性が高い。新規低分子薬および腫瘍を標的化する抗体の開発を含む、癌治療の多くのアプローチが試みられている。
移植臓器の免疫拒絶反応を検出するために、これらの方法を用いることができる。臓器移植は医療の不可欠な部分になっており、米国では年間25,000件を超える固形臓器(腎臓、肝臓、心臓、膵臓、および肺)移植および15,000件を超える骨髄移植が行われている。これらは一般に、三次医療センターで行われる複雑な手技である。移植拒絶反応のリスクを最小限に抑えるために、患者は多くの場合に長期にわたって免疫抑制の状態に置かれ、癌および感染症のリスクに曝される。さらに、多くの移植片は急性的にまたは移植の何年も後に拒絶される。これらの問題にもかかわらず、臓器不全患者にはほかに選択肢がほとんどないため、臓器移植は依然として不可欠な治療様式である。
これらの方法は、特に感染症が活動状態および潜伏状態で存在し得る場合の、感染症の治療を導く上で有用性を有する。過去一世紀にわたる感染症の治療に対する抗生物質の出現は、平均余命に大きな影響を及ぼした。過去10年の間、分子診断技法は、感染症の診断および管理において急増する役割を果たしてきた。核酸増幅によって提供される優れた感度および特異度により、これらの技法の適用はその数が増加し得た。適用の多くは、感染性病原体の存在または非存在の診断的評価に用いられる。例えば、性感染症の検査は多くの場合、核酸増幅技法を使用する分子検査によって行われる。別の一連の適用は、感染性病原体が既に診断された患者における感染の「量」の評価を含む。この例は、エイズと既に診断された患者におけるHIVウイルス量の評価である。この検査は、医師が患者の疾患がいずれの状態であるかを判定するのを助け、ひいては用いられる治療レジメンの有効性についての助言を提供し得る。
これらの方法は、高齢者における免疫系の状態をモニターする上で有用性を有する。高齢者は、感染に応答する能力、およびワクチンに対して効果的な応答を生じる能力(Weinberger et al., 2008)に影響する、免疫老化と称される免疫系の衰えを被る。これは、高齢者では肺炎による死亡率が高いこと(Office for National Statistics, 2005)、ならびにクロストリジウム・ディフィシル(Clostridium difficile)およびメチシリン耐性黄色ブドウ球菌(Staphylococcus aureus)などの院内感染への高齢者の感受性(Health Protection Agency, 2008)から明らかである。さらに、免疫系の能力の低下は、高齢者における癌罹患率の増加を説明すると考えられている。加えて、免疫老化は、アルツハイマー病および心疾患のような、炎症過程の重要な構成要素を伴う高齢者がかかる他の主要な疾患に寄与し得る。老年医学科の医師がワクチン接種、感染症の積極的治療、および入院に関する臨床決定を下す際に、どの個体がこれらの致命的な転帰のリスクが最も高いかを予測する能力は、老年医学科の医師にとって有用である。
これらの方法は、ワクチンの投与における有用性を有する。ワクチン接種の使用は、多くの生物の感染率の大幅な低下をもたらした。米国で年間30,000件を超える死亡例があり、健康に重大な影響を与え続けている1つの感染症はインフルエンザである。株が急速に突然変異するため、インフルエンザワクチン接種は毎年行わなければならない。本疾患の重症後遺症の大部分は高齢者で起こる。残念なことに、高齢者は免疫老化を被り、ワクチン接種に対する応答が不十分となる場合が多い。
適応免疫系は、病原体に関連する抗原に応答するように進化してきた。自己免疫疾患の場合と同様に、免疫系は場合により誤った標的を有し得る。自己免疫疾患では免疫系が自己抗原を標的するのに対して、過敏症反応では、免疫系は薬物、埃、および食物のような無害な刺激に対して応答を開始する。過敏症は非常によく見られ、米国人口の50%もが環境刺激に対するアレルギーを有し、これは機構によって引き起こされる。過敏症は4つの型に分類される。I型過敏症は即時型過敏症であり、IgEによって媒介される。II型は、細胞表面結合型抗原に結合するIgG抗体に起因する場合が多い。例えば、細胞の表面に結合する無害な薬物によって、たまたま抗薬物IgGを有する患者では、細胞がこれらの抗体の標的となり得る。III型は、組織上の抗原抗体複合体の沈着によって起こる。これは例えば、抗原の量が多く、結果として効率的に除去され得ず、代わりに血管壁に沈着する小さな免疫複合体が生じる場合に起こる。IV型過敏症は、T細胞によって媒介される遅延型過敏症である。I型およびIV型が、ヒトの健康に対して最も高い影響を及ぼす。
自己免疫疾患を有する対象における組換えDNAの配列決定
自己免疫疾患患者から血液試料を採取する。抗体コーティング磁気ビーズを用いて、血液試料からCD4+細胞およびCD8+細胞を単離する。PCRを用いて、T細胞受容体β遺伝子の完全な可変領域を増幅する。増幅断片をベクターにサブクローニングし、細菌に形質転換してDNA断片を単離する。細菌を増殖させてDNAを増幅し、ジデオキシ配列決定を用いてT細胞受容体β遺伝子の可変領域を配列決定して、クローン型を同定する。配列決定情報を用いて該患者のクローン型プロファイルを作成する。同様の方法を図1に示す。
自己免疫疾患の状態の決定
多発性硬化症の症状発現ピークを有する患者から、脳脊髄液(CSF)および血液の試料を採取する。CSFおよび血液からCD4+細胞を単離し、T細胞受容体β遺伝子のCDR3をPCRにより増幅する。増幅断片をベクターにサブクローニングし、細菌に形質転換してDNA断片を単離する。細菌を増殖させてDNAを増幅し、ジデオキシ配列決定を用いてT細胞受容体β遺伝子の可変領域を配列決定して、クローン型を同定する。配列決定情報を用いて、該患者のクローン型プロファイルを作成する。
TCRβレパートリー解析:増幅および配列決定の戦略
TCRレパートリーの増幅を調べるため、TCRβ鎖を解析する。解析は、TCRβ配列の増幅、配列決定、および解析を含む。1つのプライマー
は、Cβ1およびCβ2における共通配列に相補的であり、全48種のVセグメントを増幅することができる34種のVプライマー(表1)が存在する。Cβ1またはCβ2は、J/C結合部から10位および14位の位置において互いに異なる。Cβ1およびCβ2のプライマーは16 bpの位置で終了し、Cβ1またはCβ2に対する優先性を有さないはずである。
および
P7
は、分子の固相増幅(クラスター形成)に用いられる。1分子当たり3件の配列読み取りを行う。100 bpの第1の読み取りは、Illumina配列決定過程に適している融解温度を有するC'プライマーを用いて行う。第2の読み取りは6 bp長のみであり、単に試料タグを同定する目的のためである。これは、Illuminaタグプライマー
を用いて作成される。最後の読み取りは、配列
を有するIlluminaプライマーであるRead 2プライマーである。このプライマーを用いて、一次PCR Vプライマー配列から開始する、Vセグメントにおける100 bpの読み取りが作成される。
多重増幅はすべてのVセグメントを使用することができる。異なる配列の増幅における1つの問題は、異なる配列の相対的な増幅効率、および最終増幅物質において、異なる配列の最初の相対量が保存されることである。相対的な増幅効率は、異なるプライマー配列の異なる効率と、同じプライマーを使用する異なる配列の増幅の異なる効率に細分される。効率の差は、異なるプライマー配列に起因し得る。異なるVセグメントプライマーによって増幅される配列の相対存在量を維持する増幅を得るように、反応を最適化する。プライマーのいくつかは関連しており、よってプライマーの多くは「クロストーク」して、それと完全に一致しない鋳型を増幅する場合がある。どのプライマーがそれを増幅するかにかかわらず、同様の様式で各鋳型が増幅され得るように、条件を最適化することができる。換言すれば、2つの鋳型が存在する場合、1,000倍の増幅後に両方の鋳型はおよそ1,000倍増幅され得、鋳型の一方に関して、クロストークのために、増幅産物の半分が異なるプライマーを保有することは問題ではない。配列決定データのその後の解析において、プライマー配列は解析から除去され、よって鋳型が同等に増幅される限り、どのプライマーが増幅に用いられるかは問題ではない。
エラーを最小限に抑えるために、より高い忠実度を有する酵素を用いることができる。アッセイは、Taqポリメラーゼを用いて最適化した。AccuprimeおよびTaq高忠実度の使用を検証するために、Taqポリメラーゼ、Accuprime、またはTaq高忠実度を用いて、プライマーのプールでcDNAを増幅した。次に、各増幅物質を、34種のVプライマーのそれぞれおよび1種のCプライマーを用いた34件のリアルタイムPCRの鋳型として使用した。鋳型の相対量を定量した。Accuprime、Taq高忠実度、およびTaqにおける各鋳型の濃度間で高い相関(r2>0.95)が認められ、これらの高忠実度酵素の使用が検証された。
cDNAバックグラウンドのない標準鋳型においてプライマーのプールを用いて、最適化を行った。目的は、cDNA混合物においてこれらの結果の確証を得ることであった。再現性を示すために、2つ組でcDNAを増幅するためのオリゴのプールを使用した。2件の増幅のそれぞれにおいて、34種の産物のそれぞれを定量した。図5に示すように、再現性は良好であった。
プールしたオリゴ、および鋳型としての1つのcDNA試料を用いた6件の多重増幅を使用した。各増幅のうち3件はAccuprimeを用いて行い、別の3件は高忠実度Taqを用いて行った。各酵素を用いた2件の増幅は、初期RNA 500 ngに相当するcDNAを使用し、各酵素を用いた1件の増幅は10分の1のcDNAを使用した。6件の増幅のそれぞれについて、一次および二次PCRを行い、Illuminaプラットフォームおよび上記のスキームを用いて増幅物質を配列決定した。両側から100 bp配列を得た。下記と同じ概念を用いて、データの一次解析を行った。
IgHレパートリー解析:増幅および配列決定の戦略
TCRβとIgHにおけるCDR3の増幅の1つの違いは、IgHにおける体細胞突然変異の可能性のために、IgHの調査において、各V配列に対して複数のプライマーを使用する点である。各Vセグメントに対して3つの異なるプライマーを使用する。プライマーは、最も高い体細胞突然変異を有するCDRを回避する領域に存在する。3つの異なる増幅反応を行う。各反応において、各Vセグメントは3つのプライマーのうちの1つによって増幅され、すべて同じCセグメントプライマーを使用する。各反応におけるプライマーは、V-D結合部からおよそ同じ距離である。Vセグメントの最後の位置を0とすると、プライマーの第1セット(A)はおよそ-255の位置に3'末端を有し、第2セット(B)はおよそ-160の位置に3'末端を有し、第3セット(C)はおよそ-30の位置に3'末端を有する。いくつかのVセグメント間の相同性を考えると、全48種のVセグメントおよび多くの公知のアレル(国際免疫遺伝学情報システムhttp://imgt.cines.fr/によって定義される)を増幅するために、A、B、およびCフレームそれぞれにおいて23種、33種、および32種のプライマーが必要である。プライマーのリストを表2、3、および4に示す。
が、IgGの4つのセグメントおよび複数の公知のアレルを網羅する。TCRβ遺伝子の2段階のPCRと類似したスキームを用いる。V側では、各Vプライマー上の同じ5' 14 bpオーバーハングを使用する。二次PCRにおいて、V側では同じRead2-タグX-P7プライマーを使用する。C側では、TCRβ増幅で使用した戦略と類似の戦略を用いて、異なるIgGセグメントおよびそれらの公知のアレル間の変異を回避する。プライマー配列
は、図4に示す通り、3〜19位および21〜28位に由来し、異なるIgGアレルの少なくとも1つにおいて異なる塩基を有する20位を飛ばしたCセグメントの配列、ならびにクラスターの形成に用いられ得るP5の配列を含む。
ヒト配列データの一次解析
各患者試料について、それぞれが100 bpの対をなす末端読み取りであるおよそ100万件の高品質読み取りが得られる。これら100万件の読み取りは、100万個の細胞またはそれ以上から得られた100万個またはそれ以上のRNA分子に由来して、独立していると想定される。低品質の読み取りは排除する。
一方の末端において、配列決定用のC'セグメントプライマーを使用する。配列決定されるVセグメントの長さは、付加されたN+Pヌクレオチドの長さに依存する。付加されるヌクレオチドの平均数を考えると、約40ヌクレオチドのVセグメントが配列決定される。他方の末端では、Illumina配列決定プライマーP7を使用する。20 bpのVプライマー配列、およびそれに続く80 bpのVセグメント配列が得られる。
Cセグメント末端の配列決定には、Illuminaプライマーを使用する。配列決定されるべき最初の塩基はCセグメントプライマーであり、Cセグメントの0〜2塩基がそれに続き、次にDJ領域が続く。プライマー配列は、特定の読み取りがどのアイソタイプに属するかを同定する。すべてまたは大部分のDJ配列は、Cセグメント側からの読み取りを通して得られ得る。DJ領域は平均80 bpであると予測される。したがって、100 bpの読み取りは、Cセグメントプライマーおよび平均DJ領域を包含する。DJ領域によっては120 bpほどの大きさである場合もあり、それらの完全な読み取りは、(同じIgH中に2つのDセグメントが認められる場合を抜きにして)V領域からの配列決定データを含み得る。
SLE患者試料におけるTCRおよびIgHレパートリー解析
第一に、患者において疾患活動性と相関するクローン型が存在するかどうかを試験する。第二に、疾患と相関するクローン型と相関しないクローン型を識別する一連の配列特徴および/または細胞表面マーカーを明らかにする。第三に、短期(例えば、3カ月)転帰との相関など、クローン型解析が臨床的に有用な情報を提供する程度を測定する。
2つの主要な課題が存在する:相関クローン型を同定すること、およびそれらのレベルから疾患活動性を測定すること。臨床設定において、各患者について2段階でこれらの課題を行うことができる:
1) 較正試験を行い、特定の患者について相関クローン型の独自性を決定することができる。これは、相関クローン型レベルが最高レベルに達し得る症状発現のピーク時の各患者について、IgHおよびTCRβ RNA(または単一細胞に由来する連結されたTCRα-TCRβ配列)を配列決定することにより行うことができる。
2) モニタリング試験を行い、較正試験後の時点で相関クローン型のレベルを測定することができる。これは、IgHおよびTCRβ RNAを配列決定し、同じ患者の較正試料において同定された特異的相関クローン型のレベルを測定することにより行うことができる。相関クローン型のレベルを用いて、これらの時点の疾患活動性を計算する。
疾患に関連するクローン型は疾患活動性が高い時点で増加すると予測される。しかしながら、疾患活動性が高い時点で濃縮されたすべてのクローン型が、必ずしも疾患と相関するわけではない。例えば、特定の患者では、疾患活動性が高い時点で濃縮されたクローン型が10種存在し得るが、5種のみが疾患と相関する。これらの関連クローン型を同定するために、疾患と明らかに相関するクローン型のサブセット、および疾患と明らかに相関しない別のセットを調べる。クローン型のこれら2つのクラスを識別する特徴を調べる。
1) 配列モチーフ:モチーフは、相関するクローン型と関連する特異的なVもしくはJ領域、組み合わせVJ、またはDJ領域内の短い配列であってよい。
2) クローン型のサイズ。
3) レベル:絶対レベル(100万個当たりの読み取りの数)または順位レベル。
4) 他のクローン型との類似性:サイレント変化(同じアミノ酸をコードするヌクレオチドの違い)を有するもの、または保存的アミノ酸変化を有するもののような、他の高度に関連したクローン型の存在。
5) BCRに関して、クローン型における体細胞突然変異のレベル、および/またはいくつかの生殖系列クローン型と体細胞突然変異によって異なる別個のクローン型の数。
上記の項では、相関クローン型の特徴を同定するためのクローン型に基づく解析を記載した。加えて、その解析では、全HPCの一部のみを用いて、クローン型を相関的または非相関的として明らかに指定した。この項では、AutoImm(AI)スコアと称される疾患活動性の尺度を計算することを目的とした、患者レベルでの解析を記載する。上記の項を通して開発されたアルゴリズムを適用して、全HPCの中から相関クローン型を同定する。これらの相関HPCのレベルを測定する。相関クローン型のレベルを、TCRクローン型の総数に対して、および疾患と相関しないと予測されるHPCに対して正規化することができる。異なる時点におけるこれらの相関クローン型のレベルを用いて、これらの異なる時点のAIスコアを計算する。
縦断的解析では、2つの一般的疑問を評価する:ある調査点のAIスコアは同時点の疾患活動性を予測するか、およびある調査点のAIスコアは、例えば3カ月後の次の調査点といった、後の時点の疾患活動性を予測するか。
疾患活動性マーカーの予測能を最大化することができる。したがって、他のマーカーと統合したTCR/BCRレパートリー情報の予測能を試験する。これらのマーカーには、抗ds DNAおよびC3レベルのような、診療所で用いられる標準的なマーカーが含まれる。これには、公表されている他のマーカーもまた含まれる。例えば一連のケモカインは、用いられる患者と同じ1組の患者を使用して、いくらかの予測能を有することが既に示されている。この一連のものにより、TCRおよびBCRレパートリーの予測能が増大するかどうかを評価する。第1段階は、AIスコアとさらなる尺度を統合して、拡大AI(EAI)スコアを作成することである。統合を行うための様々な方法を評価することができ、EAIと3カ月後のSLEDAIとの相関の最大化により、これを最適化することができる。交差検定設計を用いて、過剰適合の程度を評価および制御する。EAIを用いて、GCとPCを識別する、および疾患活動性の変化を予測するその能力によって、3カ月後の疾患活動性を予測する能力を評価する。疾患活動性および疾患活動性の変化の測定における性能を、上記のようにROC解析を通して表すことができる。
試験する変数の数は、試料数と比較して多い。これは、最初は有望であるが、後の研究において検証され得ない結果を伴う過剰適合に結びつき得る。過剰適合のある程度の限度を得るために、訓練において交差検定アプローチを用いる。しかしながら、独立した1組の試料における検証は後の研究に関与する。これはこの提唱の要素ではないが、この指標は臨床的に適用可能であり得る。上記で得られたデータを用いて、AI、MAI、またはEAIが検証されるかどうか、および関心対象の尺度を計算するための特定の方法を決定することができる。検証には1つの特定のアルゴリズムを使用する。加えて、1つまたは複数の特定の終点を規定する。3カ月後のGCとPCを識別する能力においてAIの感度および特異度を評価して、AIが疾患活動性を予測する能力を評価することができる。別の例では、特定のRel-AI-diff閾値を用いて、3カ月内の有意な疾患活動性変化を予測するAIの感度および特異度を評価することができる。
薬物治療に対するSLE患者の反応の測定
提供する本発明の方法を用いて、薬物治療に対するSLE患者の反応を測定する。重篤な副作用を伴う高価な薬物を投与されているSLE患者がその薬物に反応しているかどうかの判定は、患者ケアにおいて、およびまたそのようなケアの管理を費用効率的にする上で役割を果たす。疾患活動性の多くの臨床的指標は治療に対して、不正確に、かつ最長数カ月という時間差の後に反応する。この期間に、疾患は進行する可能性があり、副作用によって治療に複雑さが加わる可能性がある。薬物反応を即座に理解することにより、患者はより効果的な治療により迅速に切り替えることができるようになる。
SLE患者に対する治療を漸減または中止するのに適した時点の決定
提供する本発明の方法を用いて、SLE患者に対する治療を漸減または中止するのに適した時点を決定することができる。疾患活動性の臨床的尺度によって示され得る時間差に加えて、さらなる困難はこれらの測定の感度の欠如にある。治療があまりにも早く漸減される場合、無症候性疾患はそれでもなお疾患の再度の再燃を招き得る。この結果として、免疫抑制治療の過程は典型的に、平均的な患者にとって再度の再燃のリスクが低いことを確実にするために、平均的な患者に必要な期間よりもはるかに長く、さらになお分布の末尾にとって十分長くあり得る期間行われる。したがって、副作用およびコストをもたらす顕著な過剰治療が大部分の患者において行われ、一方で一部の患者の過少治療が行われて、潜在的に予防可能な再度の再燃が起こる。再度の再燃のリスクを予測する、無症候性活動性を測定し得る方法により、設計による過剰治療に依存する代わりにそのような尺度に基づいて、治療を漸減できるようになる。
SLE患者における再燃の予測
SLE患者の治療における1つの課題は、何の兆候もなく再燃が起こり、そのため疾患を予防的に治療しようという医師の努力が打ち砕かれるという事実によって表される。再燃が起こるのを待ってから治療を開始することで、患者は潜在的に破壊的な臨床症状に曝され、高額でかつ不便な入院が必要となりかねず、それ自体副作用を伴う積極的治療介入を必要としつつ、起こるべき長期の器官損傷が生じ得る。なおさらに望ましいパラダイムは、無症候期に再燃が検出され、その時に先を見越して著しい苦痛を取り除く治療が患者に施され得、結果として入院費用が安くなり、最終的に患者にとってより良好な長期予後が可能となる治療パラダイムである。
SLE患者の自覚症状を評価するための客観的尺度
SLEは多くの器官を侵し、健常集団において非常によく見られるものを含む多くの潜在的症状を生じる。例えば、SLE患者が頭痛を訴える場合、頭痛はCNSループスの徴候である可能性があり、または一般的頭痛に起因し得る。同様に、SLE患者がある期間にわたり疲労悪化を訴えた場合、この疲労悪化は患者の疾患の憎悪に起因する可能性があり、または鬱もしくは他の原因に起因し得る。疾患活動性を反映する客観的尺度を利用できることは、SLE患者の管理に非常に役立ち得る。
MS患者の薬物治療に対する反応の測定
上記のように、MS治療における主要課題の1つは、患者が薬物治療にいかに良好に反応するか、および患者が薬物治療に反応するかどうかを測定することである。進行期および後期疾患中には、疾患によって起こった身体障害の程度を測定する総合障害度評価スコア(EDSS)などの臨床的評価が存在する。しかしながら、これらの評価は早期疾患または再発/寛解型疾患では有用ではない。疾患進行を評価するために再発周囲の臨床的パラメータを用いることができるが、患者は再発間に数年を費やすことができ、その期間中に臨床的評価から証拠はほとんど収集され得ないため、これらは荒くかつ遅行的な指標である。最後に、脳病変を調べるために、ガドリニウム増強MRIのような脳画像診断を用いることができる。MS患者は典型的に、年1回の頻度でMRIなどを受ける。しかしながら、そのような画像は特異性を欠いている。さらに、総合的な脳損傷の尺度として、それらは現在の疾患活動性の優れた尺度ではなく、病歴および脳に及ぼすその影響を反映する。
患者プロファイル:30歳の女性が、痛みを伴う単眼視力障害で来院する。患者は、神経学的評価、およびクローン性T細胞が存在するかどうかを評価するために用いられる脳脊髄液を採取するための腰椎穿刺を受ける。患者はまた、脳MRIを指示される。これらの検査に基づいて、MSとの診断が下される。患者は、1日おきに自己皮下投与すべき、1回の注射当たり250 mcgのBetaseronを処方される。6カ月後の経過観察来院時に、患者は鬱および体重増加を訴える。さらなる神経学的事象は医師に報告されていない。医師は現在、臨床的ジレンマに直面している。医師は、行われていた通りに治療を維持すべきか? 新たな治療を使用すべきか? 医師は、コストが発生し、かつ患者をさらなる造影剤曝露に曝すMRIを指示すべきか? 医師は、次回予定されているMRIから新たな病変が示されるまで待つべきか? 医師は、再燃が再発するかどうかを認めるまで待つべきか? これらの決断はすべて、疾患が活動性であるかまたはそうでないかの明白な尺度から恩恵を受ける。
MS再燃の予測
すべての自己免疫疾患と同様に、再燃の改善が治療の主要目的である。再燃は患者を衰弱させ、かつ治療するのに高価であるばかりでなく、各再燃が長期の非可逆的疾患進行に寄与するということがますます信じられている。初期再燃を管理するために、IVメチルプレドニゾロンまたは経口プレドニゾンなどのいくつかの治療を用いることができる。そのような薬物は重大な副作用があり、したがって活動性再燃の証拠なしには処方されない。より短くかつ損傷の少ない再燃を引き起こし得るこの種の先を見越した再燃治療の情報を提供するために、その後の臨床的再燃と相関した無症候性活動性の上昇の尺度を用いることができる。加えて、非常に重篤でかつ致命的な副作用のリスクを伴う、再燃の軽減に関して高い臨床的有効性を実証する治療が存在する。1つのそのような薬物は、臨床転帰の改善をもたらし、かつPMLなどの致死的脳感染症のリスクを増大させることが示されているTysabriである。これらのリスクにより、そのような薬物の価値は、他の薬物がもはや進行の制御を提供しない場合の最終治療にまで下がり、また長期的治療としてのこれらの薬物の価値は制限された。そのような薬物は、致死的副作用のリスクを最小限に抑えつつ急性再燃期を制御するよう、ステロイド剤と同様の様式で使用することができるため、再燃状態が初期である時点で予測ができる試験は、そのような薬物の有用性を増大させることができる。
実施例11による患者はBetaseronを3年間使用しており、1週間持続する臨床的再燃を報告する。年末の患者のMRIから、顕著な新たな病変が示される(複数の分離した様々なサイズの卵形の垂直方向T2WおよびFLAIR高信号病変(斑)、脳梁-中隔界面を含む、両側性の脳室周囲および皮質下白質領域を侵している、T1W画像における等低信号およびT2W画像における高信号の出現)。医師は、次の12カ月の過程にわたり患者が再燃のリスクが高いことを懸念する。臨床的ジレンマが起こる。医師は、付加的な治療を介入するために、さらなる臨床症状を待つか? 医師は治療を切り替えるべきか? もしそうするのであれば、copaxoneなどの別のクラスの注射剤を使用すべきか、またはTysabriなどの新たなクラスの治療を使用すべきか? ステロイド剤を処方すべきか? これらの臨床決定を下すのを助けるために、無症候性疾患活動性をモニターし、疾患が増大する時期、および再燃が起こる可能性が高い時期を示し得る試験を用いることができる。
MSの治療遵守のモニタリング
疾患の早期には臨床症状は比較的稀であるため、患者と患者の医師との接触はそれほど頻繁ではない。同時に、処方されている治療は、痛みのある反応および副作用を引き起こし得る自己注射を伴い、患者にとって高価でありかつ不便である。結果として、かなりの程度の治療レジメンの不遵守が認められ、患者と医師との接触が日常的ではないために、この不遵守を医師がモニターすることは難しい。無症候性疾患の状態を測定することができる試験により、医師および患者の両方が、基礎疾患がどれほど良好に制御されているかを日常的に見ることが可能になる。そのような方法は、治療を続行するようにHIV患者を効果的に動機づける点で、そのような患者において非常に効果的であることが判明している。3カ月ごとに行われる血液検査により、医師が、患者を診察し、疾患の状態を測定することが可能になる。
マウスTCRβおよびIgH配列の増幅
ヒトに関して開発したのと同様の、マウスTCRβおよびIgHの増幅および配列決定スキームを開発する。異なる配列の増幅効率の違いを最小限に抑えるための同様の方法、ならびに添加物(spike)および5' RACE技法を用いた上記と同様の検証技法を適用する。cDNAの最小インプット量を、ヒト試料について記載したのと同様の方法論において決定する。マウスとヒトの増幅スキームにおける1つの違いは、マウスにおけるTCRβの2つのCセグメントが、J/C結合部に最も近い50 bp中に多型を全く有さないという点である。したがってスキームでは、第1段階増幅用のプライマーを25〜50位に配置し、第2段階増幅に関してはプライマーを1〜25位に配置し、このプライマーは、後者のプライマーがP5配列を含むように5'尾部を有する。異なる配列によって特異性が向上し、これは、多型のために塩基が「ループアウト」する必要がないことを除いて、ヒトにおいて用いられる戦略と類似している。
マウス配列データの一次解析
マウスデータの解析に使用する解析枠組みは、ヒトデータに関して上記したものと類似している。1つの違いは、マウス試料をヒト試料よりも浅く配列決定する点である。マウス由来の血液試料は100μlであると予測される。100μlの血液中には〜100 K個のリンパ球が存在し、よって100 K件よりもはるかに高い深さまで配列決定することによって、精度が著しく向上することはない。したがって、各マウス試料について100 K件の読み取りのみを得る。読み取り数がヒトよりもマウスで少ないにもかかわらず、マウス総血中リンパ球のより多くの画分を試料採取する。総マウスリンパ球数は、ヒトのものよりも3桁超少ないと予測される。同様に、100μlの血液は、10 mlのヒト血液を用いて得られる試料採取(0.2%)と比較した場合に、マウス血液中のリンパ球のより良好な試料採取(〜10%)を提供する。
マウスSLEモデルにおけるIgHおよびTCRレパートリー解析
SLEのマウスモデルを用いて、TCR/BCRレパートリーと疾患活動性の関係を研究する。マウスモデルは、NZM2410由来のsle1およびsle3遺伝子座を有するB6である。これらのB6.sle1.sle3(BSS)マウスは、自然発症様式でSLE様腎炎を発症する。3つの型のコホートを研究する。すべての調査点について、血液BUN、クレアチニン、および抗核自己抗体、尿タンパク、およびクレアチニンレベルを得る。血液TCR/BCRレパートリーから作成されたスコアが、腎疾患のこれらの測定された指標と良好に相関するかどうかを判定する。第1コホートは記載したヒトコホートと類似しており、この場合、腎機能評価を伴って縦断的血液試料を採取する。具体的には、BSSマウス7匹を8カ月目まで月単位で追跡する。最終的に、これらのマウスを屠殺し、血液に加えて脾臓および腎組織を解析する。対照として、B6マウス5匹を同様の様式で評価する。第2コホートは横断的であり、この場合、動物の異なるコホートを特定の時点で屠殺し、脾臓、腎臓、および血液試料をその時点で解析する。具体的には、BSSマウス5匹を毎月屠殺し、血液、脾臓、および腎組織を解析する。対照として、B6対照マウス2匹を同じ様式で評価する。最後に、第3コホートを疾患の発症後にステロイド剤で処置し、その後定期的に、腎炎評価および血液試料を得る。具体的には、4カ月齢の時点で、疾患を有するマウス20匹をステロイド剤で処置した後、次の4カ月間週2回の頻度で、TCR/BCRレパートリー解析および腎機能評価のために血液を採取する。対照としてBSSマウス5匹をプラセボで処置し、同様の様式で追跡する。すべての調査点(すなわち、異なる時点、および同じ時点の異なる組織)から、TCRおよびBCRレパートリー解析を行う。解析は、上記の通り、2段階PCR、配列決定処理、および一次データ解析を含む。
マウスSLEと相関するクローン型の同定および動態
最初に、腎機能と相関する1組のクローン型を同定する。腎機能の尺度として、尿タンパク/クレアチニン比、血清クレアチニン、またはBUNレベルを使用することができる。第1および第3コホートにおいて、各HPCクローン型の血液レベルと3つの尺度のそれぞれとの相関を評価することができる。ヒトにおいて記載したのと同様の様式で、ランダム期待値(または並べ替え検定)を超えて1つ、2つ、または全3つの腎機能尺度との高い相関を有するクローン型の数の大きな増加が存在するかどうかを評価することができる。ランダム期待値を考慮して、その閾値を上回る相関レベルを有するクローン型の10%のみが、偶然に認められる相関レベルを有すると予測される(10%偽発見)相関閾値を選択する。これらのクローン型に注目し、このセットを「相関クローン型」と定義する。
相関的および非相関的という2組のクローン型の同定後、これら2組を識別する特徴を探索する。統計的および機能的に同定された相関クローン型を用いて、個別解析および複合解析を行う。例えばクローン型のレベル、特定の配列モチーフの存在、および他の関連クローン型の配列など、ヒトにおいて調べたのと同じ種類の特徴を評価する。ヒト研究について記載した通り、過剰適合の大きなリスクが存在し、よって、交差検定技法、または別個の訓練および試験セットを使用する必要がある。
疾患活動性を測定するためのIgHおよびTCRβレパートリーの使用
上記による相関クローン型のためのアルゴリズムを適用して、コホート1および3の全試料において、それらの配列および/マーカーによって相関クローン型を同定することができる。各患者における相関クローン型のレベルを用いて、腎機能の尺度と相関するAIスコアを作成することができる。上記のように、過剰適合リスクが存在し、交差検定技法ならびに/または別個の訓練および試験セットを使用する必要がある。AIと腎機能尺度との相関を、横断的様式(全マウスのすべての調査点)で評価することができる。AIスコアが個々のマウスにおいて変化するかどうかという疑問もまた、腎機能が変化する場合に評価することができる。これは、ヒトにおいて記載したのと同様の様式で、同じ動物における高い腎機能と低い腎機能からのAIを比較することによって評価することができる。
同じ細胞に由来する配列の連結
2つの配列を同じ細胞から増幅することができ、増幅中にこれらを連結して1つの単位複製配列を形成することができる。たとえ連結された配列が他の試料に由来する配列のプールと混合されたとしても、同じ細胞中のこれら2つの配列の存在に関する情報はその後保存され得る。
図9に図示する通り、プライマー1およびプライマー2を用いて配列1を増幅することができる。プライマー2は、ゲノム配列と相補的でない5'オーバーハング配列を保有する(図9A、細線)。同様に、プライマー3およびプライマー4を用いて配列2を増幅することができる(図9A)。プライマー3は、プライマー2のオーバーハング配列と相補的な5'オーバーハング配列を保有する(図9A、点線)。この図では、2つの相補的配列を表す2つのオーバーハング(または2つの連結配列)を細線で描いている;一方の配列は実線として示され、その相補体は点線として示される。他の相補的配列は、同じ単色を有するように描いてある:配列1および2に関してそれぞれ黒色および灰色。
スキーム1(a)はスキーム1の変形であり、この場合、連結配列はプライマー2配列と同一である(図10)。プライマー1、およびプライマー上にオーバーハング配列のないプライマー2を用いて、配列1を増幅することができる(図10A)。プライマー3は、プライマー2と相補的な5'オーバーハング配列を保有する(図10A)。プライマー3およびプライマー4を用いて配列2を増幅し、配列1と相補的な連結配列を創出することができる(図10A)。他の相補的配列は、同じ色を有するように描いてある:配列1および2に関してそれぞれ黒色および灰色。
図11に示すスキーム2は、最終的な増幅がゲノムと相補的でない配列を用いて達成されることを除いて、スキーム1と同様のスキームである。このアプローチの1つの利点は、オフターゲット増幅のない増幅に理想的であるようにプライミング配列を選択することができる点である。これは、増幅されるべきゲノム配列と相補的なプライマーが理想的でない場合に役立ち得る。増幅のためにゲノムと相補的でないプライマーを用いることにより、低濃度のプライマー1〜4を使用し、オフターゲット増幅を最小限に抑えることができる。また、同数のプライマー相互作用を引き起こすことなく2対以上のプライマーを使用する多重化スキームに、スキーム2を適合化することもできる。連結されるべき配列の各対は、高濃度である必要のない独自の4つのプライマーを有する。1対の増幅プライマーは、連結された配列の対をすべて増幅することができる(図11C)。
結腸癌患者における転移性再発のモニタリング
治療可能な段階で検出される多くの癌は、患者に対する転移性腫瘍再発の継続的なリスクをなお伴う。そのような再発は、後期にかつ治療不可能な段階で検出される場合が多く、患者に致命的であり得る。そのような状況の一例は、再発結腸癌である。ますます積極的になる結腸癌スクリーニングプログラムにもかかわらず、結腸癌は米国において最もよく見られる悪性腫瘍の1つである。1年におよそ150,000名の患者が、重篤であるが治療可能な病期(病期IIおよび病期III)の結腸癌と診断される。これらの患者は、腫瘍切除とその後の化学療法の過程による治療を受ける。これらの治療は一般的に有効であるが、それにもかかわらず、これらの患者が、治療後何年かのうちに原発腫瘍の転移性再発を有するというかなりの可能性がある。例えば、病期IIIの患者の50%は手術の5年以内に再発を有する。これらの再発は(例えば、結腸または肝臓における)孤発性である場合もあれば、多発性である場合もある。いずれの場合にも、しかし特にそれらが孤発性である場合に、早期でのそれらの検出は、成功的治療(手術および/または化学療法)の機会を最大にするのに役割を果たし得る。
発見研究を行って、血液TCR(および/またはBCR)のプロファイルが与えられる場合に、再発の検出の可能性を決定することができることが考えられる。転帰が判明している患者の切除腫瘍試料および経過観察血液試料の試料を、この研究に用いることができる。これらの全試料からTCR(および/またはBCR)を配列決定することができる。相関クローン型の候補は、腫瘍試料からのTCR(および/またはBCR)データ中に存在するものである。この訓練研究において判明している転帰を考慮すれば、標準的な交差検定技法を用いて、異なるクローン型のレベルが与えられる場合にスコア(再発リスク)を作成するモデルを考案することができる。したがって、切除腫瘍(較正点)におけるクローン型の測定、および再発の監視中の後の時点における同じ患者の血液中に見出されるクローン型からのデータによって、新たな患者においてこの再発スコアを算出することができる。腫瘍データを使用することで、この解析で考慮する血液中に存在するクローン型の数が大幅に減少し得る。
腫瘍標本中に濃縮されるすべてのクローン型が、腫瘍に対する免疫応答に関連するとは限らない可能性が高い。有利な炎症状態のために局所的に拡大したリンパ球がいくらか存在する可能性がある。本発明の別の態様では、同じ試料を用いて発見研究を行うことができるが、この研究は「相関」クローン型と「非相関」クローン型を識別するパラメータを同定するために用いられる。これらのパラメータには、1) 配列モチーフ:モチーフは、相関するクローン型と関連する特異的なVもしくはJ領域、組み合わせVJ、またはDJ領域内の短い配列であってよい;2) クローン型のサイズ;3) レベル:絶対レベル(100万個当たりの読み取りの数)または順位レベル;4) 他のクローン型との類似性:サイレント変化(同じアミノ酸をコードするヌクレオチドの違い)を有するもの、または保存的アミノ酸変化を有するもののような、他の高度に関連したクローン型の存在;5) BCRに関して、クローン型における体細胞突然変異のレベル、および/またはいくつかの生殖系列クローン型と体細胞突然変異によって異なる別個のクローン型の数。6) 特定のマーカーを保有する細胞の存在が含まれ得る。次にこの研究により、所与の腫瘍試料中に存在するクローン型の特定のセットが与えられる場合に、血液中でどのクローン型が癌再発と関連している可能性が高いかを予測し得るアルゴリズムがもたらされる。次にこれらのクローン型を用いて、上記と同じ様式で再発リスクのスコアを開発することができる。
本発明の別の態様では、切除腫瘍において測定されたクローン型を用いて、まだ見られていない試料における相関クローン型を予測するモデルを作成する。このモデルはまた、上記と類似した様式で再発リスクスコアを作成するために用いることもできる。このモデルでは、再発監視を受けている新たな患者において切除癌組織中のクローン型を測定する必要はなく、所与の血液試料におけるクローン型を単に測定することによって再発リスクを評価することができる。
延長として、同じ方法論を用いて原発癌の検出を達成することができることが考えられる。原発癌であるため、関連クローン型を濃縮するために用いることができる切除された腫瘍が存在しない。しかしながら、腫瘍切除データが存在する場合でさえ、関連クローン型を同定し、最終的に癌検出の可能性のスコアを作成するためには、付加的な配列および他のパラメータを使用する必要があると考えられる。したがって、拡張して、アルゴリズムが十分に予測的である場合には、切除腫瘍からのデータなしで血液(または他の体液)から癌を検出することができる。本発明のこの態様では、原発癌の診断に先立って、患者由来の血液試料を用いた発見研究が利用できることが必要である。上記と類似の様式で、パラメータ(配列およびその他)を同定して、腫瘍に対する免疫系応答に相関するクローン型を予測することができる。次にモデルを用いて、結腸癌の進行リスクを予測する癌リスクスコアを作成することができる。次にこのアルゴリズムを新たな患者の血液試料に適用して、原発性結腸癌のリスクを測定することができる。
心臓移植患者における拒絶反応のモニタリング
臓器の供給が非常に限られているため、心臓移植は比較的珍しい手技である。世界中で毎年3,500件の心臓移植が行われている。各手技は非常に高価であり、使用される臓器は値段のつけようがない。結果として、これらの臓器を受け取る患者には極めて積極的に治療がなされる。免疫抑制剤による介入が有効であり得る時点で、提供された臓器に対する免疫反応の状態を測定する目的で、患者は臓器の炎症を測定するために定期的な心臓生検を受ける。これらの検査に基づいて、免疫抑制剤の積極的な過程が行われ得る。これらの手技にはいくつかの限界がある。侵襲的な外科的手技であるため、それらは患者に対するリスクがある。さらにそれらは高価であり、低頻度の間隔でのみ行われ得る。一連の試験遺伝子11種の発現のプロファイリングに基づいた血液に基づく検査(Allomap)は、臓器拒絶反応の検出において非常に感度が高いことが示されているが、生検の代替として用いるには十分な感度が欠如しており、むしろいつ生検を行うべきかを決定するために用いられる。本発明の1つの態様では、TCR(および/またはBCR)プロファイルを用いて、「拒絶反応」の状態を評価し、特定の時間枠内で拒絶反応の可能性を予測する拒絶リスクスコアを作成する。発見研究を行って、血液TCR(および/またはBCR)のプロファイルが与えられる場合に、拒絶反応の可能性を決定することができることが考えられる。診療所でこれを用いて、用いられている免疫抑制療法の情報を与えることができる。
本発明のこの態様では、臨床転帰が判明している、血液試料のある移植後患者の集団を使用することができる。これらの全試料からTCR(および/またはBCR)を配列決定することができ、個々のクローン型と拒絶反応転帰との相関を使用して、相関クローン型と非相関クローン型を識別することができる。続いて、それら2つのクラスのクローン型を識別するパラメータを導き出すことができる。これらのパラメータには、1) 配列モチーフ:モチーフは、相関するクローン型と関連する特異的なVもしくはJ領域、組み合わせVJ、またはDJ領域内の短い配列であってよい;2) クローン型のサイズ;3) レベル:絶対レベル(100万個当たりの読み取りの数)または順位レベル;4) 他のクローン型との類似性:サイレント変化(同じアミノ酸をコードするヌクレオチドの違い)を有するもの、または保存的アミノ酸変化を有するもののような、他の高度に関連したクローン型の存在;5) BCRに関して、クローン型における体細胞突然変異のレベル、および/またはいくつかの生殖系列クローン型と体細胞突然変異によって異なる別個のクローン型の数。6) 特定のマーカーを保有する細胞の存在が含まれ得る。研究試料が移植片の生検試料を有する場合、特にそれが活発な拒絶反応の状態にある場合には、相関および非相関クローン型を規定するための代替のまたは追加の方法が生じる。その時点では、相関クローン型の大幅な濃縮が存在することが予測される。これらと他のクローン型を識別するためのパラメータを、上記の通りに同定することができる。
別の態様では、各患者に対して較正試験を用いて、相関クローン型を同定する方法を実行することができる。本方法は、移植後に採取された最初の生検試料を含む。移植後移植片の生検材料が存在することで、生検試料からTCRを解析して、この試料中に蔓延しているクローン型によって定義される相関クローン型を同定する可能性が提供される。次にクローン型のこのセットを血液中で追跡することができ、拒絶反応の可能性についてスコアを作成する。拒絶反応の可能性を概算する拒絶反応リスクスコアを作成するために、利用可能な臨床データおよび相関クローン型のレベルを使用する、上記したものと類似の発見研究を通して、拒絶反応リスクスコアを作成するためのアルゴリズムを導き出す。
別の態様では、上記のアプローチの併用により相関クローン型の同定を達成することができる。具体的には、これは、相関クローン型を予測するためのアルゴリズムを作成するための集団研究を用いることによって達成することができる。加えて、これは、移植片生検標本および/または移植前血液試料を使用する、同じ患者からの較正データを通して達成することができる。より好ましい態様では、両アプローチ:集団構築アルゴリズムおよび個々の較正を使用して、相関クローン型を最も正確に同定する。次に、訓練セットとしての集団研究の使用を通して、これらのクローン型のレベルを用いて拒絶反応リスクスコアを作成して、拒絶反応の可能性を予測する。
ナタリズマブで治療したMS患者におけるPML感染症のモニタリング
本発明の1つの態様は、MS患者における無症候性進行性多巣性白質脳症(PML)を検出するために、TCRおよび/またはBCRプロファイルを使用する。PMLは、ミエリンを合成するオリゴデンドロサイトの死滅を介して急速進行性脱髄性疾患を引き起こす場合の多い、重症でありかつ多くの場合に致命的な疾患である。これは、集団の大部分に潜伏期として存在するJCウイルスによって起こる。免疫抑制集団(例えば、エイズ)の一部では、ウイルスが再活性化されて、この重症疾患の発症を招く。加えて、移植後患者のような、薬物の使用を通して免疫抑制されている一部の患者もまた、PMLを発症し得る。いくつかの特定の薬物は、特定の患者集団におけるPMLのリスクと関連づけられている。例えば、ナタリズマブ(Tysabri)は、多発性硬化症(MS)患者の中でのPMLの10症例を超える発症と関連づけられ、しばらくの間販売が中止された。ナタリズマブは、多発性硬化症用の他のFDA認可薬物よりも効果的であることが十分に認められるが、その使用はPML発症の恐れによって制限されている。PMLが疑われたら、患者における薬物の濃度を下げるために、プラスマフェレーシスを行うことができる。MSとPMLの症状間の重複は、場合によってPMLの検出を遅らせ得る。無症候性PMLの早期検出が緊急に必要とされる。
この場合には、アルゴリズムを作成して、PMLの出現に関連するクローン型を予測する。アルゴリズムは、疾患と相関すると見なされる1組のクローン型において訓練することができる。本発明のこの態様では、その一部が次にPMLを発症する、JCウイルスによる潜伏感染を有する患者の集団による、発見研究における血液(または他の体液)試料を使用することができる。これらの全試料からTCR(および/またはBCR)を配列決定することができ、個々のクローン型と感染病原体再活性化転帰との相関を使用して、相関クローン型と非相関クローン型を識別することができる。それら2つのクラスのクローン型を識別するパラメータを同定することができる。これらのパラメータには、1) 配列モチーフ:モチーフは、相関するクローン型と関連する特異的なVもしくはJ領域、組み合わせVJ、またはDJ領域内の短い配列であってよい;2) クローン型のサイズ;3) レベル:絶対レベル(100万個当たりの読み取りの数)または順位レベル;4) 他のクローン型との類似性:サイレント変化(同じアミノ酸をコードするヌクレオチドの違い)を有するもの、または保存的アミノ酸変化を有するもののような、他の高度に関連したクローン型の存在;5) BCRに関して、クローン型における体細胞突然変異のレベル、および/またはいくつかの生殖系列クローン型と体細胞突然変異によって異なる別個のクローン型の数。6) 特定のマーカーを保有する細胞の存在が含まれ得る。同じ感染病原体に対する免疫応答を開始している1組の患者から、相関および非相関クローン型を規定するための代替のまたは追加の方法が生じる。これらの患者において濃縮されたクローン型(特に、免疫応答前よりも顕著に高いレベルにあるクローン型)を相関的と見なすことができ、それらと他のクローン型を識別するパラメータを同定することができる。
潜伏感染の再活性化のモニタリング
別の態様では、後に潜伏および再活性化が続く急性感染期を有する感染症をモニターするために、TCRおよびBCRプロファイリングを使用することができる。そのような疾患の例には、B型肝炎およびC型肝炎ならびにヘルペスウイルスが含まれる。早期での感染症の予測が望ましい。
別の態様では、各患者に対して較正試験を用いて、相関クローン型を同定する方法を実行することができる。患者が感染病原体に対して免疫応答を開始した前の時点の、同じ患者に由来する生体試料の存在は、相関クローン型を同定するのに役立ち得る。次にクローン型のこのセットを血液中で追跡することができ、再活性化の可能性について再活性化リスクスコアを作成する。再活性化の可能性を概算する再活性化リスクスコアを作成するために、利用可能な臨床データおよび相関クローン型のカウントを使用する、上記したものと類似の発見研究を通して、スコアを作成するためのアルゴリズムを導き出す。このスコアを使用するために、急性感染期中に臨床診療において新たな患者から採取された試料。このデータを潜伏期中に採取する後の試料と共に使用して、臨床目的で再活性化リスクを測定する。
別の態様では、上記のアプローチの併用により相関クローン型の同定を達成することができる。具体的には、これは、相関クローン型を予測するためのアルゴリズムを作成するための集団研究を用いることによって達成することができる。相関クローン型は、感染症の転帰が判明している患者、および/もしくは感染病原体に対する積極的な免疫応答を有する1組の患者の集団研究から、ならびに/または感染病原体と反応するクローン型を同定するためのインビトロ実験から得ることができる。加えて、これは、関連感染病原体に対する積極的な免疫応答の時点でのより古いデータ点を使用する、同じ患者からの較正データを通して達成することができる。より好ましい態様では、両アプローチ:集団構築アルゴリズムおよび個々の較正を使用して、相関クローン型を最も正確に同定する。次に、訓練セットとしての集団研究の使用を通して、これらのクローン型のレベルを用いて再活性化リスクスコアを作成して、再活性化の可能性を予測する。このスコアを使用するために、急性感染期中に診療所において新たな患者から採取された試料をプロファイルする。このデータを潜伏期中に採取する後の試料と共に使用して、臨床目的で再活性化リスクを測定する。感染病原体の排除およびそれに対する免疫を調べるために、類似の構造を使用することができる。
免疫療法中のアレルギー反応のモニタリング
アレルギー性鼻炎は、米国人口の〜11%が罹患しているよく見られる病態である。これは典型的に、花粉または埃に対するアレルギーである。曝露を排除することは難しく、これは油断のない努力を伴う。慢性鼻炎に用いられる最も一般的な治療は、充血除去薬、抗ヒスタミン薬、および鼻用ステロイド剤である。重症例では、免疫療法が行われる。免疫療法の目的は、患者を脱感作することである。まず多くの潜在的アレルゲンによる負荷を行って、患者が反応する特異的アレルゲンを同定する。次に、維持用量が達成されるまで、数カ月〜数年の期間にわたって漸増量のアレルゲンを患者に注射し、その後数年間治療を継続する。典型的に、患者は3〜6カ月以内に症状の改善を感じることができ、それは12〜18カ月ほどと遅くなる場合もあるが、大部分の患者は治療から恩恵を受けることがないか、または再発する。緩徐な用量増加の1つの理由は、十分に脱感作される前に患者が高用量のアレルゲンを投与される場合のアナフィラキシーのリスクである。
本発明のこの態様では、臨床転帰が判明している、血液試料のある、免疫療法中のアレルギー性鼻炎患者の集団を使用することができる。これらの全試料からTCR(および/またはBCR)を配列決定することができ、個々のクローン型とアレルギー転帰との相関を使用して、相関クローン型と非相関クローン型を識別することができる。続いて、それら2つのクラスのクローン型を識別するパラメータを導き出すことができる。これらのパラメータには、1) 配列モチーフ:モチーフは、相関するクローン型と関連する特異的なVもしくはJ領域、組み合わせVJ、またはDJ領域内の短い配列であってよい;2) クローン型のサイズ;3) レベル:絶対レベル(100万個当たりの読み取りの数)または順位レベル;4) 他のクローン型との類似性:サイレント変化(同じアミノ酸をコードするヌクレオチドの違い)を有するもの、または保存的アミノ酸変化を有するもののような、他の高度に関連したクローン型の存在;5) BCRに関して、クローン型における体細胞突然変異のレベル、および/またはいくつかの生殖系列クローン型と体細胞突然変異によって異なる別個のクローン型の数。6) 特定のマーカーを保有する細胞の存在が含まれ得る。相関および非相関クローン型を規定するための代替のまたは追加の方法は、特異的アレルゲンに対して陽性である患者由来の陽性アレルギー検査材料の生検標本を使用する。アレルゲンの注射部位において、相関クローン型の大幅な濃縮が存在することが予測される。これらと他のクローン型を識別するためのパラメータを、先述の通りに同定することができる。
別の態様では、各患者に対して較正試験を用いて、相関クローン型を同定する方法を実行することができる。本方法は、患者から採取された、陽性アレルゲン反応を有する部位からの生検試料を含む。これは、患者が反応している特異的アレルゲンを決定するために行われた最初のアレルギー検査に由来してよく、または任意のさらなる治療注射の部位からの試料であってもよい。いくらかの症状発現が広がっている症例では、適切なクローン型が追跡されていることを確実にするために、これを2回以上行うことができる。これらの生検試料由来のTCRおよび/またはBCRを用いて、この試料中に蔓延しているクローン型によって定義される相関クローン型を同定することができる。次にクローン型のこのセットを血液中で追跡することができ、アレルギー反応の可能性についてスコアを作成する。アレルギー状態を評価するアレルギースコアを作成するために、利用可能な臨床データおよび相関クローン型のレベルを使用する、上記したものと類似の発見研究を通して、アレルギースコアを作成するためのアルゴリズムを導き出す。
別の態様では、上記のアプローチの併用により相関クローン型の同定を達成することができる。具体的には、これは、相関クローン型を予測するためのアルゴリズムを作成するための集団研究を用いることによって達成することができる。加えて、これは、陽性アレルギー反応を有する部位からの生検標本を使用する、同じ患者からの較正データを通して達成することができる。より好ましい態様では、両アプローチ:集団構築アルゴリズムおよび個々の較正を使用して、相関クローン型を最も正確に同定する。次に、訓練セットとしての集団研究の使用を通して、これらのクローン型のレベルを用いてアレルギースコアを作成して、アレルギーの状態を予測する。
Claims (6)
- 以下の段階を含む、個体のT細胞受容体(TCR)および/またはB細胞受容体(BCR)のレパートリーをモニターする方法:
(a) T細胞および/またはB細胞を含む個体から採取した試料の該細胞から核酸分子を増幅する段階であって、該核酸分子が、T細胞受容体遺伝子または免疫グロブリン遺伝子の相補性決定領域3(CDR3)の配列を含む、段階;
(b) 個々の増幅核酸分子を空間的に単離する段階;
(c) 該空間的に単離された個々の増幅核酸分子を可逆的終結標識ヌクレオチドを用いた合成によって配列決定して、それぞれCDR3配列の少なくとも30bpを含む少なくとも10,000件の配列読み取りを提供する段階;ならびに
(d) 該試料中のCDR3配列のレベルからT細胞受容体および/またはB細胞受容体のレパートリーをモニターする段階。 - 配列の読み込みが99.9%の信頼度と異なる場合に配列の読み取りを異なるクローン型に合体させる段階をさらに含む、請求項1記載の方法。
- 各CDR3配列が、Vセグメントを含み、増幅段階が、各Vセグメントに特異的なプライマーを用いたポリメラーゼ連鎖反応における増幅段階を含む、請求項2記載の方法。
- 各試料が、少なくとも10,000個のB細胞または少なくとも10,000個のT細胞を含む、請求項1記載の方法。
- 試料が血液である、請求項1〜4のいずれか一項記載の方法。
- 各試料が、少なくとも10,000個のB細胞または少なくとも10,000個のT細胞を含み、配列決定する段階が、少なくとも100,000件の配列読み取りを提供する、請求項1記載の方法。
Applications Claiming Priority (3)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| US11269308P | 2008-11-07 | 2008-11-07 | |
| US61/112,693 | 2008-11-07 | ||
| PCT/US2009/006053 WO2010053587A2 (en) | 2008-11-07 | 2009-11-09 | Methods of monitoring conditions by sequence analysis |
Related Child Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2015164457A Division JP6112577B2 (ja) | 2008-11-07 | 2015-08-24 | 配列解析によって病態をモニターする方法 |
Publications (3)
| Publication Number | Publication Date |
|---|---|
| JP2012508011A JP2012508011A (ja) | 2012-04-05 |
| JP2012508011A5 JP2012508011A5 (ja) | 2012-12-20 |
| JP5798926B2 true JP5798926B2 (ja) | 2015-10-21 |
Family
ID=42153463
Family Applications (2)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2011535569A Active JP5798926B2 (ja) | 2008-11-07 | 2009-11-09 | 配列解析によって病態をモニターする方法 |
| JP2015164457A Active JP6112577B2 (ja) | 2008-11-07 | 2015-08-24 | 配列解析によって病態をモニターする方法 |
Family Applications After (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2015164457A Active JP6112577B2 (ja) | 2008-11-07 | 2015-08-24 | 配列解析によって病態をモニターする方法 |
Country Status (10)
| Country | Link |
|---|---|
| US (16) | US8236503B2 (ja) |
| EP (4) | EP2719774B8 (ja) |
| JP (2) | JP5798926B2 (ja) |
| CN (2) | CN102272327B (ja) |
| AU (1) | AU2009311588B2 (ja) |
| CA (1) | CA2742380C (ja) |
| ES (2) | ES2781754T3 (ja) |
| GB (5) | GB2467704B (ja) |
| SG (1) | SG195652A1 (ja) |
| WO (1) | WO2010053587A2 (ja) |
Families Citing this family (215)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| AU2002243231A1 (en) * | 2000-11-21 | 2002-07-24 | Wake Forest University | Method of treating autoimmune diseases |
| US9424392B2 (en) | 2005-11-26 | 2016-08-23 | Natera, Inc. | System and method for cleaning noisy genetic data from target individuals using genetic data from genetically related individuals |
| US8088593B2 (en) | 2007-10-02 | 2012-01-03 | Theranos, Inc. | Modular point-of-care devices, systems, and uses thereof |
| SG187453A1 (en) | 2008-01-18 | 2013-02-28 | Harvard College | Methods of detecting signatures of disease or conditions in bodily fluids |
| US8628927B2 (en) | 2008-11-07 | 2014-01-14 | Sequenta, Inc. | Monitoring health and disease status using clonotype profiles |
| US8748103B2 (en) | 2008-11-07 | 2014-06-10 | Sequenta, Inc. | Monitoring health and disease status using clonotype profiles |
| US9394567B2 (en) | 2008-11-07 | 2016-07-19 | Adaptive Biotechnologies Corporation | Detection and quantification of sample contamination in immune repertoire analysis |
| CN102272327B (zh) | 2008-11-07 | 2015-11-25 | 赛昆塔公司 | 通过序列分析监测状况的方法 |
| US9506119B2 (en) | 2008-11-07 | 2016-11-29 | Adaptive Biotechnologies Corp. | Method of sequence determination using sequence tags |
| US8691510B2 (en) * | 2008-11-07 | 2014-04-08 | Sequenta, Inc. | Sequence analysis of complex amplicons |
| US9528160B2 (en) | 2008-11-07 | 2016-12-27 | Adaptive Biotechnolgies Corp. | Rare clonotypes and uses thereof |
| US9365901B2 (en) | 2008-11-07 | 2016-06-14 | Adaptive Biotechnologies Corp. | Monitoring immunoglobulin heavy chain evolution in B-cell acute lymphoblastic leukemia |
| WO2010083456A1 (en) | 2009-01-15 | 2010-07-22 | Imdaptive Inc. | Adaptive immunity profiling and methods for generation of monoclonal antibodies |
| US8383347B1 (en) * | 2009-05-01 | 2013-02-26 | University Of South Florida | Method of diagnosing or assessing risk for Parkinson's disease or Alzheimer's disease using TCR clonality |
| EP2446052B1 (en) * | 2009-06-25 | 2018-08-08 | Fred Hutchinson Cancer Research Center | Method of measuring adaptive immunity |
| HUE052213T2 (hu) | 2009-11-06 | 2021-04-28 | Univ Leland Stanford Junior | Grafitkilökõdés nem invazív diagnosztizálása szervátültetett betegekben |
| US9043160B1 (en) | 2009-11-09 | 2015-05-26 | Sequenta, Inc. | Method of determining clonotypes and clonotype profiles |
| US20130053253A1 (en) * | 2010-02-22 | 2013-02-28 | Population Genetics Technologies Ltd | Region of Interest Extraction and Normalization Methods |
| US20190300945A1 (en) | 2010-04-05 | 2019-10-03 | Prognosys Biosciences, Inc. | Spatially Encoded Biological Assays |
| ES2555106T3 (es) | 2010-04-05 | 2015-12-29 | Prognosys Biosciences, Inc. | Ensayos biológicos codificados espacialmente |
| US10787701B2 (en) | 2010-04-05 | 2020-09-29 | Prognosys Biosciences, Inc. | Spatially encoded biological assays |
| WO2011139372A1 (en) | 2010-05-06 | 2011-11-10 | Sequenta, Inc. | Sequence analysis of complex amplicons |
| US9234240B2 (en) | 2010-05-07 | 2016-01-12 | The Board Of Trustees Of The Leland Stanford Junior University | Measurement and comparison of immune diversity by high-throughput sequencing |
| US11408031B2 (en) | 2010-05-18 | 2022-08-09 | Natera, Inc. | Methods for non-invasive prenatal paternity testing |
| US10316362B2 (en) | 2010-05-18 | 2019-06-11 | Natera, Inc. | Methods for simultaneous amplification of target loci |
| US11332793B2 (en) | 2010-05-18 | 2022-05-17 | Natera, Inc. | Methods for simultaneous amplification of target loci |
| US9677118B2 (en) | 2014-04-21 | 2017-06-13 | Natera, Inc. | Methods for simultaneous amplification of target loci |
| US11939634B2 (en) | 2010-05-18 | 2024-03-26 | Natera, Inc. | Methods for simultaneous amplification of target loci |
| CA2798758C (en) | 2010-05-18 | 2019-05-07 | Natera, Inc. | Methods for non-invasive prenatal ploidy calling |
| US11326208B2 (en) | 2010-05-18 | 2022-05-10 | Natera, Inc. | Methods for nested PCR amplification of cell-free DNA |
| US11339429B2 (en) | 2010-05-18 | 2022-05-24 | Natera, Inc. | Methods for non-invasive prenatal ploidy calling |
| US11332785B2 (en) | 2010-05-18 | 2022-05-17 | Natera, Inc. | Methods for non-invasive prenatal ploidy calling |
| US11322224B2 (en) | 2010-05-18 | 2022-05-03 | Natera, Inc. | Methods for non-invasive prenatal ploidy calling |
| US20190010543A1 (en) | 2010-05-18 | 2019-01-10 | Natera, Inc. | Methods for simultaneous amplification of target loci |
| CN101921874B (zh) * | 2010-06-30 | 2013-09-11 | 深圳华大基因科技有限公司 | 基于Solexa测序法的检测人类乳头瘤病毒的方法 |
| US20120053073A1 (en) | 2010-07-23 | 2012-03-01 | President And Fellows Of Harvard College | Methods for Detecting Signatures of Disease or Conditions in Bodily Fluids |
| MX2013000917A (es) | 2010-07-23 | 2013-07-05 | Harvard College | Metodos para detectar las enfermedades o condiciones usando celulas fagociticas. |
| CA2806293A1 (en) | 2010-07-23 | 2012-01-26 | President And Fellows Of Harvard College | Methods of detecting autoimmune or immune-related diseases or conditions |
| CA2806304A1 (en) | 2010-07-23 | 2012-01-26 | President And Fellows Of Harvard College | Methods of detecting prenatal or pregnancy-related diseases or conditions |
| EP2601521B1 (en) * | 2010-08-06 | 2018-05-02 | Ludwig-Maximilians-Universität München | Identification of t cell target antigens |
| WO2012027503A2 (en) * | 2010-08-24 | 2012-03-01 | Fred Hutchinson Cancer Research Center | Method of measuring adaptive immunity |
| CN101967476B (zh) * | 2010-09-21 | 2012-11-14 | 深圳华大基因科技有限公司 | 一种基于接头连接的DNA PCR-Free标签文库构建方法 |
| CN102409043B (zh) * | 2010-09-21 | 2013-12-04 | 深圳华大基因科技服务有限公司 | 高通量低成本Fosmid文库构建的方法及其所使用标签和标签接头 |
| CN102409045B (zh) * | 2010-09-21 | 2013-09-18 | 深圳华大基因科技服务有限公司 | 一种基于dna接头连接的标签文库构建方法及其所使用标签和标签接头 |
| CN102409044B (zh) * | 2010-09-21 | 2014-05-07 | 深圳华大基因科技服务有限公司 | 用于数字基因表达谱的标签及其使用方法 |
| CN102409408B (zh) * | 2010-09-21 | 2013-08-07 | 深圳华大基因科技服务有限公司 | 一种利用微量基因组dna进行全基因组甲基化位点精确检测的方法 |
| WO2012048340A2 (en) * | 2010-10-08 | 2012-04-12 | President And Fellows Of Harvard College | High-throughput immune sequencing |
| US9193997B2 (en) | 2010-12-15 | 2015-11-24 | The Board Of Trustees Of The Leland Stanford Junior University | Measuring and monitoring of cell clonality |
| DK2652155T3 (en) | 2010-12-16 | 2017-02-13 | Gigagen Inc | Methods for Massive Parallel Analysis of Nucleic Acids in Single Cells |
| CN103797366A (zh) * | 2011-01-14 | 2014-05-14 | Cb生物技术公司 | 免疫多样性评估方法及其用途 |
| CN111982829A (zh) | 2011-01-21 | 2020-11-24 | 拉布拉多诊断有限责任公司 | 样品使用最大化的系统和方法 |
| GB201106254D0 (en) | 2011-04-13 | 2011-05-25 | Frisen Jonas | Method and product |
| KR102039751B1 (ko) | 2011-05-31 | 2019-11-01 | 바이오젠 엠에이 인코포레이티드 | Pml의 위험을 판단하는 방법 |
| US20140235474A1 (en) | 2011-06-24 | 2014-08-21 | Sequenom, Inc. | Methods and processes for non invasive assessment of a genetic variation |
| WO2013016226A1 (en) * | 2011-07-22 | 2013-01-31 | Metamark Genetics, Inc. | Quality control method for digital pathology |
| US10385475B2 (en) | 2011-09-12 | 2019-08-20 | Adaptive Biotechnologies Corp. | Random array sequencing of low-complexity libraries |
| US9664702B2 (en) | 2011-09-25 | 2017-05-30 | Theranos, Inc. | Fluid handling apparatus and configurations |
| US20140170735A1 (en) | 2011-09-25 | 2014-06-19 | Elizabeth A. Holmes | Systems and methods for multi-analysis |
| US9619627B2 (en) | 2011-09-25 | 2017-04-11 | Theranos, Inc. | Systems and methods for collecting and transmitting assay results |
| US9632102B2 (en) | 2011-09-25 | 2017-04-25 | Theranos, Inc. | Systems and methods for multi-purpose analysis |
| US9268915B2 (en) | 2011-09-25 | 2016-02-23 | Theranos, Inc. | Systems and methods for diagnosis or treatment |
| US8475739B2 (en) | 2011-09-25 | 2013-07-02 | Theranos, Inc. | Systems and methods for fluid handling |
| JP6198736B2 (ja) * | 2011-09-22 | 2017-09-20 | リネアージュ バイオサイエンシズ, インコーポレイテッド | 疾患のシグネチャとしてのアイソタイププロファイルの検出 |
| US9250229B2 (en) | 2011-09-25 | 2016-02-02 | Theranos, Inc. | Systems and methods for multi-analysis |
| US9810704B2 (en) | 2013-02-18 | 2017-11-07 | Theranos, Inc. | Systems and methods for multi-analysis |
| US10012664B2 (en) | 2011-09-25 | 2018-07-03 | Theranos Ip Company, Llc | Systems and methods for fluid and component handling |
| US10424394B2 (en) | 2011-10-06 | 2019-09-24 | Sequenom, Inc. | Methods and processes for non-invasive assessment of genetic variations |
| US9984198B2 (en) | 2011-10-06 | 2018-05-29 | Sequenom, Inc. | Reducing sequence read count error in assessment of complex genetic variations |
| WO2013052907A2 (en) | 2011-10-06 | 2013-04-11 | Sequenom, Inc. | Methods and processes for non-invasive assessment of genetic variations |
| US9367663B2 (en) | 2011-10-06 | 2016-06-14 | Sequenom, Inc. | Methods and processes for non-invasive assessment of genetic variations |
| US10196681B2 (en) | 2011-10-06 | 2019-02-05 | Sequenom, Inc. | Methods and processes for non-invasive assessment of genetic variations |
| US8688388B2 (en) | 2011-10-11 | 2014-04-01 | Sequenom, Inc. | Methods and processes for non-invasive assessment of genetic variations |
| CA2853088C (en) | 2011-10-21 | 2018-03-13 | Adaptive Biotechnologies Corporation | Quantification of adaptive immune cell genomes in a complex mixture of cells |
| US20140336059A1 (en) * | 2011-12-05 | 2014-11-13 | Sequenta, Inc. | Clonotypes as biometric specimen tags |
| JP2015501644A (ja) * | 2011-12-09 | 2015-01-19 | シーケンタ インコーポレイテッド | 免疫活性化を測定する方法 |
| US9824179B2 (en) | 2011-12-09 | 2017-11-21 | Adaptive Biotechnologies Corp. | Diagnosis of lymphoid malignancies and minimal residual disease detection |
| US9499865B2 (en) | 2011-12-13 | 2016-11-22 | Adaptive Biotechnologies Corp. | Detection and measurement of tissue-infiltrating lymphocytes |
| WO2013096798A2 (en) * | 2011-12-22 | 2013-06-27 | Ibis Biosciences, Inc. | Amplification of a sequence from a ribonucleic acid |
| CN103184216B (zh) * | 2011-12-27 | 2015-03-18 | 深圳华大基因科技有限公司 | 用于扩增免疫球蛋白重链cdr3编码序列的引物组合物及其用途 |
| US9823246B2 (en) | 2011-12-28 | 2017-11-21 | The Board Of Trustees Of The Leland Stanford Junior University | Fluorescence enhancing plasmonic nanoscopic gold films and assays based thereon |
| EP2805280B1 (en) | 2012-01-20 | 2022-10-05 | Sequenom, Inc. | Diagnostic processes that factor experimental conditions |
| JP6302847B2 (ja) * | 2012-03-05 | 2018-03-28 | アダプティヴ バイオテクノロジーズ コーポレーション | 頻度が一致したサブユニットからの、対をなす免疫受容体鎖の決定 |
| US20150038346A1 (en) * | 2012-03-05 | 2015-02-05 | Sequenta, Inc. | Monitoring immune responsiveness to cancer vaccination |
| AU2013246050B2 (en) * | 2012-04-13 | 2017-03-16 | Adaptive Biotechnologies Corp. | Detection and quantitation of sample contamination in immune repertoire analysis |
| PL2831276T3 (pl) * | 2012-05-08 | 2016-10-31 | Kompozycje i sposób oznaczania i kalibracji dla odchylenia amplifikacji w reakcjach multipleksowej pcr | |
| US10504613B2 (en) | 2012-12-20 | 2019-12-10 | Sequenom, Inc. | Methods and processes for non-invasive assessment of genetic variations |
| US9920361B2 (en) | 2012-05-21 | 2018-03-20 | Sequenom, Inc. | Methods and compositions for analyzing nucleic acid |
| CN104520443A (zh) * | 2012-06-11 | 2015-04-15 | 赛昆塔公司 | 使用序列标签的序列确定方法 |
| WO2013188772A1 (en) * | 2012-06-14 | 2013-12-19 | Gigagen, Inc. | Methods for antibody and cell therapeutic discovery |
| AU2013273987B2 (en) * | 2012-06-15 | 2018-08-09 | Adaptive Biotechnologies Corporation | Uniquely tagged rearranged adaptive immune receptor genes in a complex gene set |
| WO2013190086A1 (en) * | 2012-06-21 | 2013-12-27 | Philip Morris Products S.A. | Systems and methods for generating biomarker signatures |
| US10497461B2 (en) | 2012-06-22 | 2019-12-03 | Sequenom, Inc. | Methods and processes for non-invasive assessment of genetic variations |
| EP2870264A4 (en) * | 2012-07-03 | 2016-03-02 | Sloan Kettering Inst Cancer | QUANTITATIVE ASSESSMENT OF THE RECOVERY OF HUMAN T-CELL REPERTOIR AFTER TRANSPLANTATION OF ALLOGENIC BLOOD-GENERATING STEM CELLS |
| AU2013293240A1 (en) * | 2012-07-24 | 2015-03-05 | Adaptive Biotechnologies Corp. | Single cell analysis using sequence tags |
| WO2014038622A1 (ja) * | 2012-09-05 | 2014-03-13 | 国立大学法人大阪大学 | 自己免疫疾患のバイオマーカー |
| WO2014055561A1 (en) | 2012-10-01 | 2014-04-10 | Adaptive Biotechnologies Corporation | Immunocompetence assessment by adaptive immune receptor diversity and clonality characterization |
| US10482994B2 (en) | 2012-10-04 | 2019-11-19 | Sequenom, Inc. | Methods and processes for non-invasive assessment of genetic variations |
| UA118441C2 (uk) | 2012-10-08 | 2019-01-25 | Протена Біосаєнсиз Лімітед | Антитіло, що розпізнає альфа-синуклеїн |
| KR101525584B1 (ko) * | 2012-12-03 | 2015-06-03 | 주식회사 케이티 | 바이오 데이터 검증 방법 및 이를 위한 장치 |
| US9265458B2 (en) | 2012-12-04 | 2016-02-23 | Sync-Think, Inc. | Application of smooth pursuit cognitive testing paradigms to clinical drug development |
| US9708514B2 (en) | 2012-12-14 | 2017-07-18 | 3M Innovative Properties Company | Method of polymerizing ethylenically-unsaturated materials using ionizing radiation |
| WO2014093141A1 (en) | 2012-12-14 | 2014-06-19 | 3M Innovative Properties Company | Method of making packaged viscoelastic compositions by polymerizing ethylenically-unsaturated materials using ionizing radiation |
| EP2746405B1 (en) * | 2012-12-23 | 2015-11-04 | HS Diagnomics GmbH | Methods and primer sets for high throughput PCR sequencing |
| US9128861B2 (en) | 2013-01-17 | 2015-09-08 | Personalis, Inc. | Methods and systems for genetic analysis |
| US20130309666A1 (en) | 2013-01-25 | 2013-11-21 | Sequenom, Inc. | Methods and processes for non-invasive assessment of genetic variations |
| US9909180B2 (en) | 2013-02-04 | 2018-03-06 | The Board Of Trustees Of The Leland Stanford Junior University | Measurement and comparison of immune diversity by high-throughput sequencing |
| KR102228488B1 (ko) * | 2013-02-11 | 2021-03-15 | 씨비 바이오테크놀로지스, 인크. | 면역 레퍼토리를 평가하기 위한 방법 |
| US11585814B2 (en) | 2013-03-09 | 2023-02-21 | Immunis.Ai, Inc. | Methods of detecting prostate cancer |
| EP2965077B1 (en) | 2013-03-09 | 2022-07-13 | Harry Stylli | Methods of detecting cancer |
| US9380976B2 (en) | 2013-03-11 | 2016-07-05 | Sync-Think, Inc. | Optical neuroinformatics |
| US10450595B2 (en) * | 2013-03-15 | 2019-10-22 | Theranos Ip Company, Llc | Nucleic acid amplification |
| AU2014233150A1 (en) * | 2013-03-15 | 2015-09-17 | Theranos Ip Company, Llc | Nucleic acid amplification |
| GB2584364A (en) | 2013-03-15 | 2020-12-02 | Abvitro Llc | Single cell bar-coding for antibody discovery |
| JP6431895B2 (ja) * | 2013-03-15 | 2018-12-05 | アダプティブ バイオテクノロジーズ コーポレイション | 複合遺伝子セットにおいてユニークにタグ付けされた再構成された適応免疫受容体遺伝子 |
| AU2014233152A1 (en) | 2013-03-15 | 2015-09-17 | Theranos Ip Company, Llc | Nucleic acid amplification |
| CA2906824C (en) | 2013-03-15 | 2023-10-03 | Theranos, Inc. | Nucleic acid amplification |
| DK2970959T3 (en) | 2013-03-15 | 2018-08-06 | Lineage Biosciences Inc | METHODS AND COMPOSITIONS FOR MARKING AND ANALYSIS OF SAMPLES |
| LT2981921T (lt) | 2013-04-03 | 2023-02-27 | Sequenom, Inc. | Neinvazinio genetinių variacijų vertinimo būdai ir procesai |
| CA2908361C (en) * | 2013-04-17 | 2023-09-26 | Pioneer Hi-Bred International, Inc. | Methods for characterizing dna sequence composition in a genome |
| EP3004383B1 (en) | 2013-05-24 | 2019-04-24 | Sequenom, Inc. | Methods for non-invasive assessment of genetic variations using area-under-curve (auc) analysis |
| MX2015016911A (es) | 2013-06-21 | 2016-06-21 | Sequenom Inc | Metodos y procesos para evaluacion no invasiva de variaciones geneticas. |
| WO2014210225A1 (en) | 2013-06-25 | 2014-12-31 | Prognosys Biosciences, Inc. | Methods and systems for determining spatial patterns of biological targets in a sample |
| US9708657B2 (en) | 2013-07-01 | 2017-07-18 | Adaptive Biotechnologies Corp. | Method for generating clonotype profiles using sequence tags |
| US9951131B2 (en) | 2013-07-12 | 2018-04-24 | Prothena Biosciences Limited | Antibodies that recognize IAPP |
| US9850302B2 (en) | 2013-07-12 | 2017-12-26 | Prothena Biosciences Limited | Antibodies that recognize IAPP |
| EP3965111A1 (en) | 2013-08-30 | 2022-03-09 | Personalis, Inc. | Methods and systems for genomic analysis |
| SG11201601611WA (en) * | 2013-09-06 | 2016-04-28 | Theranos Inc | Systems and methods for detecting infectious diseases |
| JP2016532876A (ja) | 2013-09-06 | 2016-10-20 | セラノス, インコーポレイテッド | 拭い取りを受け取るための機器、システム、方法及びキット |
| GB2535066A (en) | 2013-10-03 | 2016-08-10 | Personalis Inc | Methods for analyzing genotypes |
| CA3205430A1 (en) | 2013-10-04 | 2015-04-09 | Sequenom, Inc. | Methods and processes for non-invasive assessment of genetic variations |
| US10438691B2 (en) | 2013-10-07 | 2019-10-08 | Sequenom, Inc. | Non-invasive assessment of chromosome alterations using change in subsequence mappability |
| US20160258025A1 (en) * | 2013-10-18 | 2016-09-08 | The Regents Of The University Of California | Predicting patient responsiveness to immune checkpoint inhibitors |
| JP6220222B2 (ja) * | 2013-10-28 | 2017-10-25 | シスメックス株式会社 | 関節リウマチの診断を補助するための方法、システム及びコンピュータプログラム製品 |
| US11203783B2 (en) | 2013-11-21 | 2021-12-21 | Repertoire Genesis Incorporation | T cell receptor and B cell receptor repertoire analysis system, and use of same in treatment and diagnosis |
| WO2015134787A2 (en) | 2014-03-05 | 2015-09-11 | Adaptive Biotechnologies Corporation | Methods using randomer-containing synthetic molecules |
| WO2015138746A1 (en) * | 2014-03-12 | 2015-09-17 | The Board Of Trustees Of The Leland Stanford Junior University | Monitoring immunocompetance using immune repertoire sequencing |
| US10066265B2 (en) | 2014-04-01 | 2018-09-04 | Adaptive Biotechnologies Corp. | Determining antigen-specific t-cells |
| US11390921B2 (en) | 2014-04-01 | 2022-07-19 | Adaptive Biotechnologies Corporation | Determining WT-1 specific T cells and WT-1 specific T cell receptors (TCRs) |
| JP6744856B2 (ja) | 2014-04-08 | 2020-08-19 | プロセナ・バイオサイエンシズ・リミテッド | α−シヌクレインを認識する抗体を含む血液脳関門シャトル |
| ES2777529T3 (es) | 2014-04-17 | 2020-08-05 | Adaptive Biotechnologies Corp | Cuantificación de genomas de células inmunitarias adaptativas en una mezcla compleja de células |
| RU2717641C2 (ru) | 2014-04-21 | 2020-03-24 | Натера, Инк. | Обнаружение мутаций и плоидности в хромосомных сегментах |
| US10202640B2 (en) | 2014-05-07 | 2019-02-12 | The Board Of Trustees Of The Leland Stanford Junior University | Single cell analysis of T cells using high-throughput multiplex amplification and deep sequencing |
| CN113249435A (zh) * | 2014-06-26 | 2021-08-13 | 10X基因组学有限公司 | 分析来自单个细胞或细胞群体的核酸的方法 |
| US11783911B2 (en) | 2014-07-30 | 2023-10-10 | Sequenom, Inc | Methods and processes for non-invasive assessment of genetic variations |
| AU2015314813B2 (en) | 2014-09-11 | 2022-02-24 | Immunis.Ai, Inc. | Methods of detecting prostate cancer |
| EP3194593B1 (en) | 2014-09-15 | 2019-02-06 | AbVitro LLC | High-throughput nucleotide library sequencing |
| CA2966201A1 (en) | 2014-10-29 | 2016-05-06 | Adaptive Biotechnologies Corp. | Highly-multiplexed simultaneous detection of nucleic acids encoding paired adaptive immune receptor heterodimers from many samples |
| EP4026913A1 (en) | 2014-10-30 | 2022-07-13 | Personalis, Inc. | Methods for using mosaicism in nucleic acids sampled distal to their origin |
| WO2016073778A2 (en) | 2014-11-05 | 2016-05-12 | Nirmidas Biotech, Inc. | Metal composites for enhanced imaging |
| US10246701B2 (en) | 2014-11-14 | 2019-04-02 | Adaptive Biotechnologies Corp. | Multiplexed digital quantitation of rearranged lymphoid receptors in a complex mixture |
| EP3224384A4 (en) | 2014-11-25 | 2018-04-18 | Adaptive Biotechnologies Corp. | Characterization of adaptive immune response to vaccination or infection using immune repertoire sequencing |
| AU2016222788B2 (en) | 2015-02-24 | 2022-03-31 | Adaptive Biotechnologies Corp. | Methods for diagnosing infectious disease and determining HLA status using immune repertoire sequencing |
| WO2016161273A1 (en) | 2015-04-01 | 2016-10-06 | Adaptive Biotechnologies Corp. | Method of identifying human compatible t cell receptors specific for an antigenic target |
| EP3901281B1 (en) | 2015-04-10 | 2022-11-23 | Spatial Transcriptomics AB | Spatially distinguished, multiplex nucleic acid analysis of biological specimens |
| CN107849560B (zh) | 2015-04-27 | 2021-10-22 | 阿布维特罗有限责任公司 | 对治疗剂和疾病特异性抗原进行测序、确定、配对和验证的方法 |
| US11479812B2 (en) | 2015-05-11 | 2022-10-25 | Natera, Inc. | Methods and compositions for determining ploidy |
| US9422547B1 (en) | 2015-06-09 | 2016-08-23 | Gigagen, Inc. | Recombinant fusion proteins and libraries from immune cell repertoires |
| JP6576129B2 (ja) * | 2015-07-06 | 2019-09-18 | キヤノン株式会社 | 通信装置、通信方法およびプログラム |
| US10539564B2 (en) | 2015-07-22 | 2020-01-21 | Roche Sequencing Solutions, Inc. | Identification of antigen epitopes and immune sequences recognizing the antigens |
| EP3325646B1 (en) | 2015-07-22 | 2020-08-19 | F.Hoffmann-La Roche Ag | Identification of antigen epitopes and immune sequences recognizing the antigens |
| AU2016321333A1 (en) * | 2015-09-09 | 2018-04-26 | Psomagen, Inc. | Method and system for microbiome-derived diagnostics and therapeutics for conditions associated with cerebro-craniofacial health |
| CA3006036A1 (en) * | 2015-09-09 | 2017-03-16 | uBiome, Inc. | Method and system for microbiome-derived diagnostics and therapeutics for eczema |
| WO2017132438A1 (en) * | 2016-01-29 | 2017-08-03 | The Johns Hopkins University | Bottleneck sequencing |
| WO2017165614A1 (en) * | 2016-03-23 | 2017-09-28 | The Methodist Hospital System | Pre-transplant tcr clonality assessment to predict post-liver transplant survival |
| US11299783B2 (en) | 2016-05-27 | 2022-04-12 | Personalis, Inc. | Methods and systems for genetic analysis |
| US11774446B2 (en) | 2016-06-20 | 2023-10-03 | Cowper Sciences Inc. | Methods for diagnosis and treatment of autoimmune diseases |
| US11747334B2 (en) | 2016-06-20 | 2023-09-05 | Cowper Sciences Inc. | Methods for differential diagnosis of autoimmune diseases |
| EP3491560A1 (en) | 2016-07-27 | 2019-06-05 | Sequenom, Inc. | Genetic copy number alteration classifications |
| US10676736B2 (en) | 2016-08-05 | 2020-06-09 | Bio-Rad Laboratories, Inc. | Second strand direct |
| US10428325B1 (en) | 2016-09-21 | 2019-10-01 | Adaptive Biotechnologies Corporation | Identification of antigen-specific B cell receptors |
| US11485996B2 (en) | 2016-10-04 | 2022-11-01 | Natera, Inc. | Methods for characterizing copy number variation using proximity-litigation sequencing |
| WO2018089858A1 (en) | 2016-11-11 | 2018-05-17 | Healthtell Inc. | Methods for identifying candidate biomarkers |
| US10011870B2 (en) | 2016-12-07 | 2018-07-03 | Natera, Inc. | Compositions and methods for identifying nucleic acid molecules |
| US10550429B2 (en) | 2016-12-22 | 2020-02-04 | 10X Genomics, Inc. | Methods and systems for processing polynucleotides |
| CN110249060A (zh) | 2017-01-17 | 2019-09-17 | 生命技术公司 | 用于免疫组库测序的组合物和方法 |
| US11694768B2 (en) | 2017-01-24 | 2023-07-04 | Sequenom, Inc. | Methods and processes for assessment of genetic variations |
| CN110612119A (zh) | 2017-02-07 | 2019-12-24 | 西雅图儿童医院(Dba西雅图儿童研究所) | 磷脂醚(ple)car t细胞肿瘤靶向(ctct)剂 |
| EP3589295A4 (en) | 2017-02-28 | 2020-11-04 | Endocyte, Inc. | COMPOSITIONS AND METHODS OF T CAR LYMPHOCYTE THERAPY |
| US10822662B2 (en) | 2017-03-06 | 2020-11-03 | Karkinos Precision Oncology LLC | Diagnostic methods for identifying T-cell lymphoma and leukemia by high-throughput TCR-β sequencing |
| CN108728903A (zh) * | 2017-04-21 | 2018-11-02 | 深圳市乐土精准医疗科技有限公司 | 基于高通量测序用于地中海贫血大样本筛查的建库方法 |
| US20180315510A1 (en) * | 2017-04-27 | 2018-11-01 | Koninklijke Philips N.V. | Use of clinical knowledge to improve use of next generation sequencing |
| US11754552B2 (en) * | 2017-06-09 | 2023-09-12 | The Regents Of The University Of California | Use of immune repertoire diversity for predicting transplant rejection |
| WO2018237075A1 (en) | 2017-06-20 | 2018-12-27 | The Medical College Of Wisconsin, Inc. | ASSESSING THE RISK OF GRAFT COMPLICATION WITH TOTAL ACELLULAR DNA |
| US10636512B2 (en) | 2017-07-14 | 2020-04-28 | Cofactor Genomics, Inc. | Immuno-oncology applications using next generation sequencing |
| EP3431610A1 (en) | 2017-07-19 | 2019-01-23 | Noscendo GmbH | Methods and devices for nucleic acid-based real-time determination of disease states |
| CN111344416A (zh) | 2017-09-01 | 2020-06-26 | 生命技术公司 | 用于免疫组库测序的组合物和方法 |
| US11254980B1 (en) | 2017-11-29 | 2022-02-22 | Adaptive Biotechnologies Corporation | Methods of profiling targeted polynucleotides while mitigating sequencing depth requirements |
| TW201940182A (zh) | 2018-01-22 | 2019-10-16 | 美商安德賽特公司 | Car t 細胞之使用方法 |
| WO2019157529A1 (en) | 2018-02-12 | 2019-08-15 | 10X Genomics, Inc. | Methods characterizing multiple analytes from individual cells or cell populations |
| CN112005306A (zh) * | 2018-03-13 | 2020-11-27 | 格里尔公司 | 选择、管理和分析高维数据的方法和系统 |
| WO2019200410A1 (en) * | 2018-04-13 | 2019-10-17 | Freenome Holdings, Inc. | Machine learning implementation for multi-analyte assay of biological samples |
| US20210214758A1 (en) * | 2018-05-07 | 2021-07-15 | Id Genomics, Inc. | Methods and tools for determining clonal relatedness and predicting clonal traits |
| US11814750B2 (en) | 2018-05-31 | 2023-11-14 | Personalis, Inc. | Compositions, methods and systems for processing or analyzing multi-species nucleic acid samples |
| US10801064B2 (en) | 2018-05-31 | 2020-10-13 | Personalis, Inc. | Compositions, methods and systems for processing or analyzing multi-species nucleic acid samples |
| US11189361B2 (en) | 2018-06-28 | 2021-11-30 | International Business Machines Corporation | Functional analysis of time-series phylogenetic tumor evolution tree |
| US11211148B2 (en) | 2018-06-28 | 2021-12-28 | International Business Machines Corporation | Time-series phylogenetic tumor evolution trees |
| US11525159B2 (en) | 2018-07-03 | 2022-12-13 | Natera, Inc. | Methods for detection of donor-derived cell-free DNA |
| EP3894593A2 (en) | 2018-12-13 | 2021-10-20 | DNA Script | Direct oligonucleotide synthesis on cells and biomolecules |
| CN109554440A (zh) * | 2018-12-26 | 2019-04-02 | 山东艾克韦生物技术有限公司 | 多重引物组及利用该引物组基于高通量测序构建人类t细胞免疫组库的方法 |
| CN109593758B (zh) * | 2018-12-26 | 2021-11-26 | 山东艾克韦生物技术有限公司 | 多重引物组及利用该引物组基于高通量测序构建人类b细胞免疫组库的方法 |
| WO2020191365A1 (en) | 2019-03-21 | 2020-09-24 | Gigamune, Inc. | Engineered cells expressing anti-viral t cell receptors and methods of use thereof |
| US11931674B2 (en) | 2019-04-04 | 2024-03-19 | Natera, Inc. | Materials and methods for processing blood samples |
| EP4010902A4 (en) * | 2019-08-05 | 2023-08-23 | Tata Consultancy Services Limited | MULTIPLE SCLEROSIS RISK ASSESSMENT SYSTEM AND METHOD |
| CN111081334B (zh) * | 2019-12-18 | 2023-04-18 | 鲁东大学 | 一种基于风险因素概率组合分析的慢性疾病早期预警方法 |
| EP4150118A1 (en) * | 2020-05-14 | 2023-03-22 | Becton Dickinson and Company | Primers for immune repertoire profiling |
| EP4025692A2 (en) | 2020-06-02 | 2022-07-13 | 10X Genomics, Inc. | Nucleic acid library methods |
| WO2021247568A1 (en) | 2020-06-02 | 2021-12-09 | 10X Genomics, Inc. | Spatial trancriptomics for antigen-receptors |
| EP4162074B1 (en) | 2020-06-08 | 2024-04-24 | 10X Genomics, Inc. | Methods of determining a surgical margin and methods of use thereof |
| WO2022204443A1 (en) | 2021-03-24 | 2022-09-29 | Genentech, Inc. | Efficient tcr gene editing in t lymphocytes |
| WO2022266774A1 (en) * | 2021-06-25 | 2022-12-29 | Sunnybrook Research Institute | Systems and methods for characterizing intra-tumor regions on quantitative ultrasound parametric images to predict cancer response to chemotherapy at pre-treatment |
| CN113792099B (zh) * | 2021-08-12 | 2023-08-25 | 上海熙业信息科技有限公司 | 一种基于历史效用表剪枝的数据流高效用项集挖掘系统 |
| CN113822170B (zh) * | 2021-08-31 | 2024-02-06 | 西安理工大学 | 身体非静止状态的手部震颤识别方法 |
| WO2023086639A1 (en) * | 2021-11-11 | 2023-05-19 | The General Hospital Corporation | Methods for defining stages and progression of amyotrophic lateral sclerosis |
| WO2023183468A2 (en) * | 2022-03-25 | 2023-09-28 | Freenome Holdings, Inc. | Tcr/bcr profiling for cell-free nucleic acid detection of cancer |
| CN116469473B (zh) * | 2023-06-15 | 2023-09-22 | 北京智因东方转化医学研究中心有限公司 | T细胞亚型鉴定的模型训练方法、装置、设备及存储介质 |
Family Cites Families (340)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| US3270960A (en) | 1964-09-11 | 1966-09-06 | Sperry Rand Corp | Fluid sensor |
| US3773919A (en) | 1969-10-23 | 1973-11-20 | Du Pont | Polylactide-drug mixtures |
| DE3211263A1 (de) | 1981-03-31 | 1983-01-27 | Otsuka Pharmaceutical Co. Ltd., Tokyo | Human-interferon verwandte peptide, antigene und antikoerper, sowie verfahren zu deren herstellung |
| DE3238353A1 (de) | 1982-10-15 | 1984-04-19 | Max Planck Gesellschaft zur Förderung der Wissenschaften e.V., 3400 Göttingen | Verfahren zur simultanen quantitativen bestimmung der blutzellen und reagenz hierfuer |
| US5189147A (en) | 1984-06-13 | 1993-02-23 | Massachusetts Institute Of Technology | Meterodimeric T lymphocyte receptor antibody |
| US4683195A (en) | 1986-01-30 | 1987-07-28 | Cetus Corporation | Process for amplifying, detecting, and/or-cloning nucleic acid sequences |
| US4683202A (en) | 1985-03-28 | 1987-07-28 | Cetus Corporation | Process for amplifying nucleic acid sequences |
| US4965188A (en) | 1986-08-22 | 1990-10-23 | Cetus Corporation | Process for amplifying, detecting, and/or cloning nucleic acid sequences using a thermostable enzyme |
| DE3541033A1 (de) | 1985-11-19 | 1987-05-21 | Boehringer Mannheim Gmbh | Verfahren zur quantifizierung von zellpopulationen bzw. subpopulationen sowie hierfuer geeignetes reagenz |
| US4800159A (en) | 1986-02-07 | 1989-01-24 | Cetus Corporation | Process for amplifying, detecting, and/or cloning nucleic acid sequences |
| US4942124A (en) | 1987-08-11 | 1990-07-17 | President And Fellows Of Harvard College | Multiplex sequencing |
| US5149625A (en) | 1987-08-11 | 1992-09-22 | President And Fellows Of Harvard College | Multiplex analysis of DNA |
| US5667967A (en) | 1990-05-01 | 1997-09-16 | The Board Of Trustees Of The Leland Stanford Junior University | T-cell receptor varible transcripts as disease related markers |
| US5506126A (en) | 1988-02-25 | 1996-04-09 | The General Hospital Corporation | Rapid immunoselection cloning method |
| US5168038A (en) | 1988-06-17 | 1992-12-01 | The Board Of Trustees Of The Leland Stanford Junior University | In situ transcription in cells and tissues |
| US5296351A (en) * | 1988-10-20 | 1994-03-22 | Alexander A. Morley | Method for diagnosis of monoclonality in leukaemia and lymphoma |
| US5075217A (en) | 1989-04-21 | 1991-12-24 | Marshfield Clinic | Length polymorphisms in (dC-dA)n ·(dG-dT)n sequences |
| US5231012A (en) | 1989-06-28 | 1993-07-27 | Schering Corporation | Nucleic acids encoding cytokine synthesis inhibitory factor (interleukin-10) |
| CA2020958C (en) | 1989-07-11 | 2005-01-11 | Daniel L. Kacian | Nucleic acid sequence amplification methods |
| US5298396A (en) * | 1989-11-15 | 1994-03-29 | National Jewish Center For Immunology And Respiratory Medicine | Method for identifying T cells disease involved in autoimmune disease |
| US5336598A (en) * | 1989-11-15 | 1994-08-09 | National Jewish Center For Immunology And Respiratory Medicine | Method for diagnosing a superantigen caused pathologial condition via assay of T-cells |
| US5126022A (en) | 1990-02-28 | 1992-06-30 | Soane Tecnologies, Inc. | Method and device for moving molecules by the application of a plurality of electrical fields |
| US6054034A (en) | 1990-02-28 | 2000-04-25 | Aclara Biosciences, Inc. | Acrylic microchannels and their use in electrophoretic applications |
| US6916605B1 (en) | 1990-07-10 | 2005-07-12 | Medical Research Council | Methods for producing members of specific binding pairs |
| GB9015198D0 (en) | 1990-07-10 | 1990-08-29 | Brien Caroline J O | Binding substance |
| WO1992002551A1 (en) | 1990-08-02 | 1992-02-20 | B.R. Centre Limited | Methods for the production of proteins with a desired function |
| US5210015A (en) | 1990-08-06 | 1993-05-11 | Hoffman-La Roche Inc. | Homogeneous assay system using the nuclease activity of a nucleic acid polymerase |
| IE76732B1 (en) | 1990-08-07 | 1997-11-05 | Becton Dickinson Co | One step test for absolute counts |
| US5699798A (en) | 1990-08-10 | 1997-12-23 | University Of Washington | Method for optically imaging solid tumor tissue |
| US5635354A (en) * | 1991-01-09 | 1997-06-03 | Institut National De La Sante Et De La Recherche Medicale (Inserm) | Method for describing the repertoires of antibodies (Ab) and of T-cell receptors (TcR) of an individual's immune system |
| US5364759B2 (en) | 1991-01-31 | 1999-07-20 | Baylor College Medicine | Dna typing with short tandem repeat polymorphisms and identification of polymorphic short tandem repeats |
| JPH06502997A (ja) | 1991-02-12 | 1994-04-07 | ルセル ユクラフ | ヒトTリンパ球レセプターのβ鎖の可変領域をコードするヌクレオチド配列対応するペプチドセグメント並びに診断及び治療への利用 |
| JP3080178B2 (ja) | 1991-02-18 | 2000-08-21 | 東洋紡績株式会社 | 核酸配列の増幅方法およびそのための試薬キット |
| US6091000A (en) * | 1991-03-15 | 2000-07-18 | Duke University | SCID mouse engrafted with human synovium tissue |
| JP3266311B2 (ja) | 1991-05-02 | 2002-03-18 | 生化学工業株式会社 | 新規ポリペプチドおよびこれを用いる抗hiv剤 |
| US5674679A (en) | 1991-09-27 | 1997-10-07 | Amersham Life Science, Inc. | DNA cycle sequencing |
| US5981179A (en) | 1991-11-14 | 1999-11-09 | Digene Diagnostics, Inc. | Continuous amplification reaction |
| US5256542A (en) | 1992-03-09 | 1993-10-26 | Tanox Biosystems, Inc. | Selecting low frequency antigen-specific single B lymphocytes with correction for background noise |
| US5213960A (en) | 1992-03-09 | 1993-05-25 | Tanox Biosystems, Inc. | Methods for selecting low frequency antigen-specific single B lymphocytes |
| US5837447A (en) * | 1992-04-15 | 1998-11-17 | Blood Center Research Foundation, Inc., The | Monitoring an immune response by analysis of amplified immunoglobulin or T-cell-receptor nucleic acid |
| US5587128A (en) | 1992-05-01 | 1996-12-24 | The Trustees Of The University Of Pennsylvania | Mesoscale polynucleotide amplification devices |
| US5498392A (en) | 1992-05-01 | 1996-03-12 | Trustees Of The University Of Pennsylvania | Mesoscale polynucleotide amplification device and method |
| US5981176A (en) | 1992-06-17 | 1999-11-09 | City Of Hope | Method of detecting and discriminating between nucleic acid sequences |
| US5925517A (en) | 1993-11-12 | 1999-07-20 | The Public Health Research Institute Of The City Of New York, Inc. | Detectably labeled dual conformation oligonucleotide probes, assays and kits |
| JPH10504181A (ja) * | 1994-04-18 | 1998-04-28 | ニューヨーク ソサエティ フォー ザ リリーフ オブ ザ ラプチャード アンド クリップルド メインティニング ザ ホスピタル フォー スペシャル サージェリー | 保存されたt細胞レセプター配列 |
| US6001229A (en) | 1994-08-01 | 1999-12-14 | Lockheed Martin Energy Systems, Inc. | Apparatus and method for performing microfluidic manipulations for chemical analysis |
| US6090592A (en) | 1994-08-03 | 2000-07-18 | Mosaic Technologies, Inc. | Method for performing amplification of nucleic acid on supports |
| FR2724182B1 (fr) * | 1994-09-02 | 1996-12-13 | Pasteur Institut | Obtention d'un anticorps monoclonal recombinant a partir d'un anticorps monoclonal humain anti-rhesus d, sa production en cellules d'insecte, et ses utilisations |
| US5604097A (en) | 1994-10-13 | 1997-02-18 | Spectragen, Inc. | Methods for sorting polynucleotides using oligonucleotide tags |
| US5846719A (en) | 1994-10-13 | 1998-12-08 | Lynx Therapeutics, Inc. | Oligonucleotide tags for sorting and identification |
| US5776737A (en) | 1994-12-22 | 1998-07-07 | Visible Genetics Inc. | Method and composition for internal identification of samples |
| US6919434B1 (en) | 1995-02-20 | 2005-07-19 | Sankyo Co., Ltd. | Monoclonal antibodies that bind OCIF |
| US5698396A (en) * | 1995-06-07 | 1997-12-16 | Ludwig Institute For Cancer Research | Method for identifying auto-immunoreactive substances from a subject |
| WO1997013868A1 (en) | 1995-10-11 | 1997-04-17 | Leonard Adleman | Large scale dna sequencing by position sensitive hybridization |
| WO1997013877A1 (en) | 1995-10-12 | 1997-04-17 | Lynx Therapeutics, Inc. | Measurement of gene expression profiles in toxicity determination |
| US6087096A (en) * | 1995-11-13 | 2000-07-11 | Dau; Peter C. | Method of intrafamily fragment analysis of the T cell receptor α and β chain CDR3 regions |
| US5854033A (en) | 1995-11-21 | 1998-12-29 | Yale University | Rolling circle replication reporter systems |
| KR19990087749A (ko) * | 1996-03-13 | 1999-12-27 | 시오노 요시히코 | 류마티스성 관절염에 특이적인 인간 티 세포 클론 |
| US6458530B1 (en) | 1996-04-04 | 2002-10-01 | Affymetrix Inc. | Selecting tag nucleic acids |
| CA2257152C (en) * | 1996-06-03 | 2009-01-27 | Linda M. Pilarski | Methods for detection of rearranged dna |
| ATE318327T1 (de) | 1996-06-04 | 2006-03-15 | Univ Utah Res Found | Fluoreszenz-donor-akzeptor paar |
| AU3878697A (en) | 1996-06-20 | 1998-02-02 | Cornell Research Foundation Inc. | Identification of abnormalities in the expression of t and cell antigen receptors as indicators of disease diagnosis, prognosis and therapeutic predictors |
| US6074827A (en) | 1996-07-30 | 2000-06-13 | Aclara Biosciences, Inc. | Microfluidic method for nucleic acid purification and processing |
| CA2264925C (en) * | 1996-09-06 | 2010-12-07 | Alain T. Luxembourg | Purification of antigen-specific t cells |
| US5935793A (en) | 1996-09-27 | 1999-08-10 | The Chinese University Of Hong Kong | Parallel polynucleotide sequencing method using tagged primers |
| GB9626815D0 (en) * | 1996-12-23 | 1997-02-12 | Cemu Bioteknik Ab | Method of sequencing DNA |
| GB9704444D0 (en) | 1997-03-04 | 1997-04-23 | Isis Innovation | Non-invasive prenatal diagnosis |
| ES2563643T3 (es) | 1997-04-01 | 2016-03-15 | Illumina Cambridge Limited | Método de secuenciación de ácido nucleico |
| US6143496A (en) | 1997-04-17 | 2000-11-07 | Cytonix Corporation | Method of sampling, amplifying and quantifying segment of nucleic acid, polymerase chain reaction assembly having nanoliter-sized sample chambers, and method of filling assembly |
| EP1908832B1 (en) | 1997-07-07 | 2012-12-26 | Medical Research Council | A method for increasing the concentration of a nucleic acid molecule |
| US7572582B2 (en) | 1997-09-12 | 2009-08-11 | Exiqon A/S | Oligonucleotide analogues |
| US6794499B2 (en) | 1997-09-12 | 2004-09-21 | Exiqon A/S | Oligonucleotide analogues |
| US6008002A (en) | 1997-09-29 | 1999-12-28 | Bodey; Bela | Immunomagnetic detection and isolation of cancer cells |
| WO1999019717A1 (en) | 1997-10-15 | 1999-04-22 | Aclara Biosciences, Inc. | Laminate microstructure device and method for making same |
| JP2001520054A (ja) | 1997-10-23 | 2001-10-30 | エグザクト サイエンシーズ コーポレイション | Pcrを用いる分子診断におけるコンタミネーションを検出するための方法 |
| US7351578B2 (en) | 1999-12-10 | 2008-04-01 | Invitrogen Corp. | Use of multiple recombination sites with unique specificity in recombinational cloning |
| DE69941689D1 (de) | 1998-02-12 | 2010-01-07 | Univ Texas | Verfahren und reagenzien zur raschen und effizienten isolierung zirkulierender krebszellen |
| US6210910B1 (en) * | 1998-03-02 | 2001-04-03 | Trustees Of Tufts College | Optical fiber biosensor array comprising cell populations confined to microcavities |
| JP4262799B2 (ja) | 1998-04-16 | 2009-05-13 | 平田機工株式会社 | 生タイヤ供給方法 |
| DE19833738A1 (de) | 1998-07-27 | 2000-02-03 | Michael Giesing | Verfahren zur Isolierung von Krebszellen aus zellhaltigen Körperflüssigkeiten sowie Sets zur Durchführung dieses Verfahrens |
| US6787308B2 (en) | 1998-07-30 | 2004-09-07 | Solexa Ltd. | Arrayed biomolecules and their use in sequencing |
| DE19844931C1 (de) | 1998-09-30 | 2000-06-15 | Stefan Seeger | Verfahren zur DNS- oder RNS-Sequenzierung |
| AR021833A1 (es) | 1998-09-30 | 2002-08-07 | Applied Research Systems | Metodos de amplificacion y secuenciacion de acido nucleico |
| US6541608B1 (en) | 1999-02-23 | 2003-04-01 | Baylor College Of Medicine | T cell receptor Vβ-Dβ-Jβ sequence and methods for its detection |
| US6307024B1 (en) | 1999-03-09 | 2001-10-23 | Zymogenetics, Inc. | Cytokine zalpha11 Ligand |
| US6300070B1 (en) | 1999-06-04 | 2001-10-09 | Mosaic Technologies, Inc. | Solid phase methods for amplifying multiple nucleic acids |
| US6440706B1 (en) | 1999-08-02 | 2002-08-27 | Johns Hopkins University | Digital amplification |
| US20040209314A1 (en) | 1999-09-06 | 2004-10-21 | Institut National De La Sante Et De La Recherche Medicale France | Means for detection and purification of CD8+ T lymphocyte populations specific to peptides presented in the context of HLA |
| US6235483B1 (en) | 2000-01-31 | 2001-05-22 | Agilent Technologies, Inc. | Methods and kits for indirect labeling of nucleic acids |
| EP1283906A4 (en) | 2000-03-31 | 2005-04-27 | Univ Southern California | EPIGENETIC SEQUENCES FOR DININGENEROKARZINOME |
| AUPQ687600A0 (en) * | 2000-04-13 | 2000-05-11 | Flinders Technologies Pty Ltd | A method of detection |
| US20030207300A1 (en) | 2000-04-28 | 2003-11-06 | Matray Tracy J. | Multiplex analytical platform using molecular tags |
| US6596492B2 (en) * | 2000-07-11 | 2003-07-22 | Colorado State University Research Foundation | PCR materials and methods useful to detect canine and feline lymphoid malignancies |
| US7567870B1 (en) * | 2000-07-31 | 2009-07-28 | Institute For Systems Biology | Multiparameter analysis for predictive medicine |
| US6939451B2 (en) | 2000-09-19 | 2005-09-06 | Aclara Biosciences, Inc. | Microfluidic chip having integrated electrodes |
| ATE380883T1 (de) | 2000-10-24 | 2007-12-15 | Univ Leland Stanford Junior | Direkte multiplex charakterisierung von genomischer dna |
| US6778724B2 (en) | 2000-11-28 | 2004-08-17 | The Regents Of The University Of California | Optical switching and sorting of biological samples and microparticles transported in a micro-fluidic device, including integrated bio-chip devices |
| AU2002253981B2 (en) | 2001-02-20 | 2008-02-21 | Abeome Corporation | Rapid production of monoclonal antibodies |
| US7265208B2 (en) | 2001-05-01 | 2007-09-04 | The Regents Of The University Of California | Fusion molecules and treatment of IgE-mediated allergic diseases |
| US20040235061A1 (en) | 2001-05-24 | 2004-11-25 | Wilkie Bruce N. | Methods for selecting and producing animals having a predicted level of immune response, disease resistance or susceptibility, and/or productivity |
| US20050260570A1 (en) | 2001-05-29 | 2005-11-24 | Mao Jen-I | Sequencing by proxy |
| US6720144B1 (en) * | 2001-06-21 | 2004-04-13 | Quest Diagnostics | Detection of clonal T-cell receptor-γ gene rearrangement by PCR/temporal temperature gradient gel electrophoresis (TTGE) |
| US7112423B2 (en) | 2001-07-15 | 2006-09-26 | Keck Graduate Institute | Nucleic acid amplification using nicking agents |
| WO2003020983A1 (en) | 2001-08-30 | 2003-03-13 | Virginia Commonwealth University | Allele specific pcr for genotyping |
| AU2002322518A1 (en) | 2001-08-31 | 2003-03-18 | Rosetta Inpharmactis Llc | Methods for preparing nucleic acid samples |
| CA2457652C (en) | 2001-08-31 | 2012-08-07 | Avidex Limited | Soluble t cell receptor |
| JP4439262B2 (ja) * | 2001-09-19 | 2010-03-24 | アレクシオン ファーマシューティカルズ, インコーポレイテッド | 操作されたテンプレートおよび単一プライマー増幅におけるそれらの使用 |
| KR20040064275A (ko) * | 2001-11-09 | 2004-07-16 | 소스 프리시전 메디슨, 인코포레이티드 | 유전자 발현 프로파일을 이용한 질병의 동정, 모니터링,치료 및 생물학적 상태의 확인 |
| GB2382137A (en) | 2001-11-20 | 2003-05-21 | Mats Gullberg | Nucleic acid enrichment |
| GB0128153D0 (en) | 2001-11-23 | 2002-01-16 | Bayer Ag | Profiling of the immune gene repertoire |
| WO2003052101A1 (en) | 2001-12-14 | 2003-06-26 | Rosetta Inpharmatics, Inc. | Sample tracking using molecular barcodes |
| GB0130267D0 (en) | 2001-12-19 | 2002-02-06 | Neutec Pharma Plc | Focussed antibody technology |
| WO2003059155A2 (en) | 2002-01-09 | 2003-07-24 | Maxx Genetech Co. Ltd | Method of detecting t-cell proliferation for diagnosis of diseases by gene array |
| AUPS028002A0 (en) | 2002-02-01 | 2002-02-28 | Ausman Engineering And Associates Pty Ltd | A bearing assembly |
| US7157274B2 (en) | 2002-06-24 | 2007-01-02 | Cytonome, Inc. | Method and apparatus for sorting particles |
| WO2004046098A2 (en) * | 2002-05-16 | 2004-06-03 | Vanderbilt University | Method for predicting autoimmune diseases |
| US20060259248A1 (en) * | 2002-07-01 | 2006-11-16 | Institut Pasteur | System, method, device, and computer program product for extraction, gathering, manipulation, and analysis of peak data from an automated sequencer |
| WO2004005465A2 (en) * | 2002-07-03 | 2004-01-15 | Institute For Scientific Research, Inc. | Compositions and methods for the detection of human t cell receptor variable family gene expression |
| DE60334474D1 (de) | 2002-07-12 | 2010-11-18 | Univ Johns Hopkins | Reagenzien und verfahren zum eingriff in einzigartige klonotype lymphozyten-rezeptoren |
| WO2004009765A2 (en) | 2002-07-19 | 2004-01-29 | Althea Technologies, Inc. | Strategies for gene expression analysis |
| US7157228B2 (en) | 2002-09-09 | 2007-01-02 | Bioarray Solutions Ltd. | Genetic analysis and authentication |
| US7459273B2 (en) | 2002-10-04 | 2008-12-02 | Affymetrix, Inc. | Methods for genotyping selected polymorphism |
| US8859748B2 (en) | 2002-10-11 | 2014-10-14 | Jacobus Johannes Maria van Dongen | Nucleic acid amplification primers for PCR-based clonality studies |
| US20050009096A1 (en) | 2002-10-11 | 2005-01-13 | The Regents Of The University Of California | Method for diagnosis and prognosis of multiple sclerosis |
| WO2004044209A1 (en) | 2002-11-13 | 2004-05-27 | Monoquant Pty Ltd | A method of detection |
| WO2004051266A1 (ja) * | 2002-11-14 | 2004-06-17 | Atsushi Muraguchi | 抗原特異的リンパ球検出用マイクロウェルアレイチップ、抗原特異的リンパ球の検出法及び製造方法、並びに抗原特異的リンパ球抗原受容体遺伝子のクローニング方法 |
| WO2004053104A2 (en) | 2002-12-11 | 2004-06-24 | Coley Pharmaceutical Group, Inc. | 5’ cpg nucleic acids and methods of use |
| WO2004063706A2 (en) | 2003-01-08 | 2004-07-29 | Maxx Genetech Co., Ltd. | Method of detecting over-expression of t-cell receptor genes by real-time pcr |
| EP2159285B1 (en) | 2003-01-29 | 2012-09-26 | 454 Life Sciences Corporation | Methods of amplifying and sequencing nucleic acids |
| GB0304068D0 (en) | 2003-02-22 | 2003-03-26 | Avidex Ltd | Substances |
| US20070042349A1 (en) | 2003-04-24 | 2007-02-22 | Ogle Brenda M | Methods for assessing biologic diversity |
| AU2003902299A0 (en) | 2003-05-13 | 2003-05-29 | Flinders Medical Centre | A method of analysing a marker nucleic acid molecule |
| US20070105105A1 (en) * | 2003-05-23 | 2007-05-10 | Mount Sinai School Of Medicine Of New York University | Surrogate cell gene expression signatures for evaluating the physical state of a subject |
| US20050010030A1 (en) | 2003-07-02 | 2005-01-13 | Zang Jingwu Z. | T cell receptor CDR3 sequence and methods for detecting and treating rheumatoid arthritis |
| EP2532745B1 (en) | 2003-07-05 | 2015-09-09 | The Johns Hopkins University | Method and Compositions for Detection and Enumeration of Genetic Variations |
| US20060228350A1 (en) | 2003-08-18 | 2006-10-12 | Medimmune, Inc. | Framework-shuffling of antibodies |
| US20050048498A1 (en) | 2003-08-29 | 2005-03-03 | Applera Corporation | Compositions, methods, and kits for assembling probes |
| US7365179B2 (en) | 2003-09-09 | 2008-04-29 | Compass Genetics, Llc | Multiplexed analytical platform |
| TWI333977B (en) | 2003-09-18 | 2010-12-01 | Symphogen As | Method for linking sequences of interest |
| FR2863274B1 (fr) * | 2003-12-05 | 2012-11-16 | Commissariat Energie Atomique | Procede d'evaluation quantitative d'un rearrangement ou d'une recombinaison genetique ciblee d'un individu et ses applications. |
| WO2005053603A2 (en) | 2003-12-08 | 2005-06-16 | Yeda Research And Development Co. Ltd. | Antigen receptor variable region typing |
| US20080166718A1 (en) * | 2003-12-15 | 2008-07-10 | Institut Pasteur | Repertoire determination of a lymphocyte B population |
| DE60326052D1 (de) | 2003-12-15 | 2009-03-19 | Pasteur Institut | Ermittlung des Repertoires von B-Lymphozyten Populationen |
| US20070160994A1 (en) | 2003-12-15 | 2007-07-12 | Institut Pasteur | Repertoire determination of a lymphocyte b population |
| WO2006019407A2 (en) | 2004-02-18 | 2006-02-23 | The Trustees Of Boston University | Method for detecting and quantifying rare mutations/polymorphisms |
| US20060046258A1 (en) * | 2004-02-27 | 2006-03-02 | Lapidus Stanley N | Applications of single molecule sequencing |
| US20070161001A1 (en) * | 2004-03-04 | 2007-07-12 | Dena Leshkowitz | Quantifying and profiling antibody and t cell receptor gene expression |
| JP4480423B2 (ja) * | 2004-03-08 | 2010-06-16 | 独立行政法人科学技術振興機構 | 免疫細胞クローンの拡大の有無の判定方法 |
| DE102004016437A1 (de) * | 2004-04-04 | 2005-10-20 | Oligene Gmbh | Verfahren zur Erkennung von Signaturen in komplexen Genexpressionsprofilen |
| US20050250147A1 (en) | 2004-05-10 | 2005-11-10 | Macevicz Stephen C | Digital profiling of polynucleotide populations |
| WO2006076025A2 (en) | 2004-05-14 | 2006-07-20 | Amaox, Inc. | Immune cell biosensors and methods of using same |
| EP1598429A1 (en) | 2004-05-19 | 2005-11-23 | Amplion Ltd. | Detection of amplicon contamination during PCR exhibiting two different annealing temperatures |
| GB0412973D0 (en) | 2004-06-10 | 2004-07-14 | Celltech R&D Ltd | Identification of antibody producing cells |
| US20060020397A1 (en) | 2004-07-21 | 2006-01-26 | Kermani Bahram G | Methods for nucleic acid and polypeptide similarity search employing content addressable memories |
| US20060019304A1 (en) | 2004-07-26 | 2006-01-26 | Paul Hardenbol | Simultaneous analysis of multiple genomes |
| US20060094018A1 (en) * | 2004-08-03 | 2006-05-04 | Bauer A R Jr | Discovery and a method for the early detection of pancreatic cancer and other disease conditions |
| US7820382B2 (en) * | 2004-08-03 | 2010-10-26 | Bauer A Robert | Method for the early detection of breast cancer, lung cancer, pancreatic cancer and colon polyps, growths and cancers as well as other gastrointestinal disease conditions and the preoperative and postoperative monitoring of transplanted organs from the donor and in the recipient and their associated conditions related and unrelated to the organ transplantation |
| RS51326B (sr) | 2004-08-05 | 2010-12-31 | Genentech Inc. | Humanizovani anti-cmet antagonisti |
| CA2576702C (en) | 2004-08-11 | 2016-10-04 | Albert Einstein College Of Medicine Of Yeshiva University | Isolation, gene expression, and chemotherapeutic resistance of motile cancer cells |
| US7915036B2 (en) * | 2004-09-13 | 2011-03-29 | The United States Of America As Represented By The Secretary, Department Of Health And Human Services | Compositions comprising T cell receptors and methods of use thereof |
| US7170050B2 (en) | 2004-09-17 | 2007-01-30 | Pacific Biosciences Of California, Inc. | Apparatus and methods for optical analysis of molecules |
| AU2005302425A1 (en) | 2004-10-29 | 2006-05-11 | Benaroya Research Institute At Virginia Mason | Methods of generating antigen-specific CD4+CD25+ regulatory T cells, compositions and methods of use |
| US7966988B2 (en) | 2005-01-11 | 2011-06-28 | Exxonmobil Research And Engineering Company | Method for controlling soot induced lubricant viscosity increase |
| US8029783B2 (en) | 2005-02-02 | 2011-10-04 | Genentech, Inc. | DR5 antibodies and articles of manufacture containing same |
| FR2881436B1 (fr) * | 2005-02-03 | 2007-04-27 | Commissariat Energie Atomique | Procede de determination de la diversite des lymphocytes t dans un echantillon biologique |
| US7393665B2 (en) | 2005-02-10 | 2008-07-01 | Population Genetics Technologies Ltd | Methods and compositions for tagging and identifying polynucleotides |
| AU2006214034A1 (en) * | 2005-02-16 | 2006-08-24 | Wyeth | Methods and systems for diagnosis, prognosis and selection of treatment of leukemia |
| US7537894B2 (en) | 2005-03-02 | 2009-05-26 | The University Of Chicago | Methods and kits for monitoring Barrett's metaplasia |
| WO2006099164A2 (en) | 2005-03-10 | 2006-09-21 | Applera Corporation | Methods for multiplex amplification |
| US20060211030A1 (en) | 2005-03-16 | 2006-09-21 | Sydney Brenner | Methods and compositions for assay readouts on multiple analytical platforms |
| CA2604095A1 (en) | 2005-04-12 | 2006-10-19 | 454 Life Sciences Corporation | Methods for determining sequence variants using ultra-deep sequencing |
| WO2006116155A2 (en) | 2005-04-21 | 2006-11-02 | The Regents Of The University Of California | A method for diagnosis and prognosis of multiple sclerosis subtypes |
| US20060263789A1 (en) | 2005-05-19 | 2006-11-23 | Robert Kincaid | Unique identifiers for indicating properties associated with entities to which they are attached, and methods for using |
| US7208795B2 (en) | 2005-05-24 | 2007-04-24 | Atmel Corporation | Low-cost, low-voltage single-layer polycrystalline EEPROM memory cell integration into BiCMOS technology |
| US8426146B2 (en) | 2005-06-03 | 2013-04-23 | University of Pittsburgh—of the Commonwealth System of Higher Education | Multiparameteric method for assessing immune system status |
| EP2463386B1 (en) | 2005-06-15 | 2017-04-12 | Complete Genomics Inc. | Nucleic acid analysis by random mixtures of non-overlapping fragments |
| US20070020670A1 (en) | 2005-07-07 | 2007-01-25 | Hematologics, Inc. | Methods for detecting and confirming minimal disease |
| US20070020640A1 (en) | 2005-07-21 | 2007-01-25 | Mccloskey Megan L | Molecular encoding of nucleic acid templates for PCR and other forms of sequence analysis |
| US7993821B2 (en) | 2005-08-11 | 2011-08-09 | University Of Washington | Methods and apparatus for the isolation and enrichment of circulating tumor cells |
| GB0521521D0 (en) | 2005-10-21 | 2005-11-30 | Medical Res Council | Diagnostic methods and kits |
| GB0522310D0 (en) | 2005-11-01 | 2005-12-07 | Solexa Ltd | Methods of preparing libraries of template polynucleotides |
| US20070105165A1 (en) | 2005-11-04 | 2007-05-10 | Charles Goolsby | Composite profiles of cell antigens and target signal transduction proteins for analysis and clinical management of hematologic cancers |
| US7375211B2 (en) * | 2005-11-18 | 2008-05-20 | Kou Zhong C | Method for detection and quantification of T-cell receptor Vβ repertoire |
| US8137936B2 (en) | 2005-11-29 | 2012-03-20 | Macevicz Stephen C | Selected amplification of polynucleotides |
| WO2007087312A2 (en) | 2006-01-23 | 2007-08-02 | Population Genetics Technologies Ltd. | Molecular counting |
| WO2007087310A2 (en) | 2006-01-23 | 2007-08-02 | Population Genetics Technologies Ltd. | Nucleic acid analysis using sequence tokens |
| SG10201405158QA (en) | 2006-02-24 | 2014-10-30 | Callida Genomics Inc | High throughput genome sequencing on dna arrays |
| WO2007101441A1 (en) * | 2006-03-06 | 2007-09-13 | Symphogen A/S | Recombinant polyclonal antibody for treatment of respiratory syncytial virus infections |
| ES2546848T3 (es) | 2006-03-10 | 2015-09-29 | Epigenomics Ag | Un método para identificar una muestra biológica para el análisis de la metilación |
| EP2002017B1 (en) * | 2006-04-04 | 2015-06-10 | Keygene N.V. | High throughput detection of molecular markers based on restriction fragments |
| EP2021460A4 (en) | 2006-05-11 | 2010-11-17 | Univ Maryland Biotech Inst | GENERAL PROCEDURE FOR GENERATING HUMAN ANTIBODY REACTIONS IN VITRO |
| WO2007136518A2 (en) * | 2006-05-17 | 2007-11-29 | Torrey Pines Institute For Molecular Studies | Treatment of autoimmune disorders |
| US20090208955A1 (en) | 2006-05-25 | 2009-08-20 | Institute For Advance Study | Methods for identifying sequence motifs, and applications thereof |
| US7833716B2 (en) | 2006-06-06 | 2010-11-16 | Gen-Probe Incorporated | Tagged oligonucleotides and their use in nucleic acid amplification methods |
| CN101467082B (zh) | 2006-06-12 | 2011-12-14 | 加利福尼亚太平洋生物科学公司 | 实施分析反应的基材 |
| US20100027896A1 (en) | 2006-06-28 | 2010-02-04 | Amir Geva | Automated application interaction using a virtual operator |
| WO2008005673A2 (en) * | 2006-06-30 | 2008-01-10 | Applera Corporation | Reversible terminator nucleotides and methods of use |
| WO2008108803A2 (en) | 2006-07-13 | 2008-09-12 | Amaox, Ltd. | Immune cell biosensors and methods of using same |
| US8394590B2 (en) | 2006-08-02 | 2013-03-12 | California Institute Of Technology | Capture agents and related methods and systems for detecting and/or sorting targets |
| US20080274904A1 (en) * | 2006-08-10 | 2008-11-06 | Niall Anthony Gormley | Method of target enrichment |
| WO2008026927A2 (en) | 2006-08-30 | 2008-03-06 | Academisch Medisch Centrum | Process for displaying t- and b-cell receptor repertoires |
| WO2008039694A2 (en) | 2006-09-26 | 2008-04-03 | St. Jude Children's Research Hospital | Methods and compositions for monitoring t cell receptor diversity |
| US8088379B2 (en) | 2006-09-26 | 2012-01-03 | The United States Of America As Represented By The Department Of Health And Human Services | Modified T cell receptors and related materials and methods |
| JP5026047B2 (ja) * | 2006-10-18 | 2012-09-12 | 株式会社膠原病研究所 | 自己免疫疾患の発症に関わる自己応答性t細胞またはt細胞受容体の同定方法、およびその利用 |
| US8148067B2 (en) * | 2006-11-09 | 2012-04-03 | Xdx, Inc. | Methods for diagnosing and monitoring the status of systemic lupus erythematosus |
| US8262900B2 (en) | 2006-12-14 | 2012-09-11 | Life Technologies Corporation | Methods and apparatus for measuring analytes using large scale FET arrays |
| US7862999B2 (en) | 2007-01-17 | 2011-01-04 | Affymetrix, Inc. | Multiplex targeted amplification using flap nuclease |
| PT2121920E (pt) * | 2007-03-01 | 2011-10-03 | Symphogen As | Método de clonagem de anticorpos cognatos |
| WO2008147879A1 (en) | 2007-05-22 | 2008-12-04 | Ryan Golhar | Automated method and device for dna isolation, sequence determination, and identification |
| EP2164985A4 (en) | 2007-06-01 | 2014-05-14 | 454 Life Sciences Corp | SYSTEM AND METHOD FOR IDENTIFYING INDIVIDUAL SAMPLES FROM A MULTIPLEX MIXTURE |
| WO2009015296A1 (en) | 2007-07-24 | 2009-01-29 | The Regents Of The University Of California | Microfabricated dropley generator |
| CA2693979A1 (en) | 2007-07-26 | 2009-02-05 | Pacific Biosciences Of California, Inc. | Molecular redundant sequencing |
| ITRM20070429A1 (it) | 2007-08-06 | 2009-02-07 | Uni Cattolica Del Sacro Cuor E | Mezzi per la diagnosi la prevenzione e la cura dell'artrite reumatoide. |
| WO2009021215A1 (en) | 2007-08-09 | 2009-02-12 | Celula, Inc. | Methods and devices for correlated, multi-parameter single cell measurements and recovery of remnant biological material |
| US8268564B2 (en) * | 2007-09-26 | 2012-09-18 | President And Fellows Of Harvard College | Methods and applications for stitched DNA barcodes |
| WO2009045898A2 (en) | 2007-09-28 | 2009-04-09 | Mayo Foundation For Medical Education And Research | Assessing t cell repertoires |
| US7960116B2 (en) | 2007-09-28 | 2011-06-14 | Pacific Biosciences Of California, Inc. | Nucleic acid sequencing methods and systems |
| JP5730576B2 (ja) | 2007-11-07 | 2015-06-10 | ジェネンテック, インコーポレイテッド | 抗cd40抗体による治療に対するb細胞リンパ腫の応答性を評価するための方法及び組成物 |
| WO2009070767A2 (en) | 2007-11-28 | 2009-06-04 | Whitehead Institute For Biomedical Research | Systemic instigation systems to study tumor growth or metastasis |
| EP2062982A1 (fr) | 2007-11-26 | 2009-05-27 | ImmunID | Procédé d'étude de la diversité combinatoire V(D)J |
| CN101225441B (zh) | 2007-12-05 | 2010-12-01 | 浙江大学 | 一种检测克隆特异性t淋巴细胞tcr bv cdr3基因组成的方法 |
| US20100021894A1 (en) * | 2007-12-20 | 2010-01-28 | Northwestern University | Nanoparticle-Based Colorimetric Detection Of Cysteine |
| US8621502B2 (en) | 2007-12-21 | 2013-12-31 | Microsoft Corporation | Obtaining user reactions to video |
| US11051733B2 (en) | 2008-01-18 | 2021-07-06 | Wake Forest University Health Sciences | Isolating and purifying cells for therapy |
| US7767400B2 (en) * | 2008-02-03 | 2010-08-03 | Helicos Biosciences Corporation | Paired-end reads in sequencing by synthesis |
| EP2088432A1 (en) | 2008-02-11 | 2009-08-12 | MorphoSys AG | Methods for identification of an antibody or a target |
| EP2088205A1 (en) | 2008-02-11 | 2009-08-12 | Institut National De La Sante Et De La Recherche Medicale (Inserm) | PSMB10: A diagnosis marker and therapeutic target of chronic rejection. |
| WO2009108866A2 (en) | 2008-02-28 | 2009-09-03 | The Ohio State University Research Foundation | Microrna signatures associated with cytogenetics and prognosis in acute myeloid leukemia (aml) and uses thereof |
| US20110054009A1 (en) | 2008-02-28 | 2011-03-03 | The Ohio State University Research Foundation | MicroRNA-Based Methods and Compositions for the Diagnosis, Prognosis and Treatment of Prostate Related Disorders |
| US20090226975A1 (en) * | 2008-03-10 | 2009-09-10 | Illumina, Inc. | Constant cluster seeding |
| TW200938840A (en) | 2008-03-12 | 2009-09-16 | Emo Biomedicine Corp | A method for in vitro study of immune modulation using pig blood cell |
| EP2100970B1 (en) * | 2008-03-13 | 2017-05-10 | National Institute of Immunology | Ig genes specific oligonucleotides and uses thereof |
| CN104862383B (zh) | 2008-03-28 | 2019-05-28 | 加利福尼亚太平洋生物科学股份有限公司 | 用于核酸测序的组合物和方法 |
| ATE530497T1 (de) | 2008-03-31 | 2011-11-15 | Sony Deutschland Gmbh | Verfahren zur herstellung einer membran mit konischer pore |
| DK2281065T3 (en) * | 2008-04-16 | 2015-10-05 | Hudsonalpha Inst For Biotechnology | PROCEDURE TO EVALUATE AND COMPARE IMMUNE REPERTOIRS |
| US8911948B2 (en) | 2008-04-30 | 2014-12-16 | Integrated Dna Technologies, Inc. | RNase H-based assays utilizing modified RNA monomers |
| EP2277049A4 (en) | 2008-05-09 | 2012-05-30 | Univ Duke | AUTOANTIBODIES IN THE DETECTION AND TREATMENT OF CANCER |
| US9068181B2 (en) | 2008-05-23 | 2015-06-30 | The General Hospital Corporation | Microfluidic droplet encapsulation |
| DE102008025656B4 (de) | 2008-05-28 | 2016-07-28 | Genxpro Gmbh | Verfahren zur quantitativen Analyse von Nukleinsäuren, Marker dafür und deren Verwendung |
| US20110124520A1 (en) | 2008-05-30 | 2011-05-26 | Massachuesetts Institute Of Technology | Compositions and Methods for Spatial Separation and Screening of Cells |
| WO2009151628A2 (en) | 2008-06-12 | 2009-12-17 | Gov't Of The Usa, As Represented By The Secretary, Department Of Health Human Services | Monitoring tcr-b to determine hiv therapy and disease progression |
| AU2009262112A1 (en) | 2008-06-25 | 2009-12-30 | Baylor Research Institute | Blood transcriptional signature of mycobacterium tuberculosis infection |
| WO2010011894A1 (en) | 2008-07-24 | 2010-01-28 | The Board Of Regents Of The University Of Texas System | Vh4 codon signature for multiple sclerosis |
| EP2316030B1 (en) * | 2008-07-25 | 2019-08-21 | Wagner, Richard W. | Protein screeing methods |
| US9156010B2 (en) * | 2008-09-23 | 2015-10-13 | Bio-Rad Laboratories, Inc. | Droplet-based assay system |
| GB2477053B (en) | 2008-09-23 | 2013-11-13 | Quantalife Inc | Droplet-based assay system |
| US8699361B2 (en) | 2008-09-30 | 2014-04-15 | Qualcomm Incorporated | Out-of-synchronization handling method and apparatus |
| US8546128B2 (en) | 2008-10-22 | 2013-10-01 | Life Technologies Corporation | Fluidics system for sequential delivery of reagents |
| US20100137143A1 (en) | 2008-10-22 | 2010-06-03 | Ion Torrent Systems Incorporated | Methods and apparatus for measuring analytes |
| JP2012507726A (ja) | 2008-10-31 | 2012-03-29 | クゥアルコム・インコーポレイテッド | 測位システムにおける磁気計の使用 |
| US8748103B2 (en) | 2008-11-07 | 2014-06-10 | Sequenta, Inc. | Monitoring health and disease status using clonotype profiles |
| US9506119B2 (en) | 2008-11-07 | 2016-11-29 | Adaptive Biotechnologies Corp. | Method of sequence determination using sequence tags |
| US9394567B2 (en) | 2008-11-07 | 2016-07-19 | Adaptive Biotechnologies Corporation | Detection and quantification of sample contamination in immune repertoire analysis |
| US9528160B2 (en) | 2008-11-07 | 2016-12-27 | Adaptive Biotechnolgies Corp. | Rare clonotypes and uses thereof |
| US8691510B2 (en) * | 2008-11-07 | 2014-04-08 | Sequenta, Inc. | Sequence analysis of complex amplicons |
| CN102272327B (zh) | 2008-11-07 | 2015-11-25 | 赛昆塔公司 | 通过序列分析监测状况的方法 |
| US9365901B2 (en) | 2008-11-07 | 2016-06-14 | Adaptive Biotechnologies Corp. | Monitoring immunoglobulin heavy chain evolution in B-cell acute lymphoblastic leukemia |
| US8628927B2 (en) | 2008-11-07 | 2014-01-14 | Sequenta, Inc. | Monitoring health and disease status using clonotype profiles |
| US20140234835A1 (en) | 2008-11-07 | 2014-08-21 | Sequenta, Inc. | Rare clonotypes and uses thereof |
| WO2010060051A2 (en) | 2008-11-21 | 2010-05-27 | Emory University | Systems biology approach predicts the immunogenicity of vaccines |
| US8367330B2 (en) | 2008-12-22 | 2013-02-05 | Quest Diagnostics Investments Incorporated | Methods for detecting TCR-gamma gene rearrangement |
| EP2384367A4 (en) | 2008-12-30 | 2013-07-10 | Janssen Biotech Inc | SERUM MARKERS TO PREDICT THE CLINICAL RESPONSE TO ANTI-TNF ANTIBODIES IN PATIENTS WITH MORBUS BECHTEREW |
| WO2010083456A1 (en) | 2009-01-15 | 2010-07-22 | Imdaptive Inc. | Adaptive immunity profiling and methods for generation of monoclonal antibodies |
| CN102333891A (zh) * | 2009-01-20 | 2012-01-25 | 利兰·斯坦福青年大学托管委员会 | 用于药靶诊断、预后和鉴别的单细胞基因表达 |
| US20100323348A1 (en) | 2009-01-31 | 2010-12-23 | The Regents Of The University Of Colorado, A Body Corporate | Methods and Compositions for Using Error-Detecting and/or Error-Correcting Barcodes in Nucleic Acid Amplification Process |
| US8673627B2 (en) | 2009-05-29 | 2014-03-18 | Life Technologies Corporation | Apparatus and methods for performing electrochemical reactions |
| US8574835B2 (en) | 2009-05-29 | 2013-11-05 | Life Technologies Corporation | Scaffolded nucleic acid polymer particles and methods of making and using |
| EP2446052B1 (en) * | 2009-06-25 | 2018-08-08 | Fred Hutchinson Cancer Research Center | Method of measuring adaptive immunity |
| EP2278513A1 (en) * | 2009-07-15 | 2011-01-26 | Nagravision SA | Method for preventing the use of a cloned user unit communicating with a server |
| JP5829606B2 (ja) | 2009-06-29 | 2015-12-09 | カリフォルニア・インスティテュート・オブ・テクノロジーCalifornia Institute Oftechnology | 単一細胞からの未知の再配列されたt細胞受容体の単離 |
| CN102575292B (zh) | 2009-09-22 | 2015-07-29 | 霍夫曼-拉罗奇有限公司 | 与疾病相关的kir单元型的测定 |
| US9043160B1 (en) | 2009-11-09 | 2015-05-26 | Sequenta, Inc. | Method of determining clonotypes and clonotype profiles |
| US9315857B2 (en) | 2009-12-15 | 2016-04-19 | Cellular Research, Inc. | Digital counting of individual molecules by stochastic attachment of diverse label-tags |
| US8835358B2 (en) | 2009-12-15 | 2014-09-16 | Cellular Research, Inc. | Digital counting of individual molecules by stochastic attachment of diverse labels |
| US8545248B2 (en) | 2010-01-07 | 2013-10-01 | Life Technologies Corporation | System to control fluid flow based on a leak detected by a sensor |
| KR101323827B1 (ko) | 2010-01-08 | 2013-10-31 | 키스트 유럽 에프게엠베하 | 강직성척추염 진단용 프라이머 및 이를 이용한 강직성 척추염 진단 방법 |
| GB201000375D0 (en) | 2010-01-09 | 2010-02-24 | Univ Cardiff | T Cell clonotypes |
| WO2011106738A2 (en) | 2010-02-25 | 2011-09-01 | Fred Hutchinson Cancer Research Center | Use of tcr clonotypes as biomarkers for disease |
| EP2367000A1 (en) | 2010-03-04 | 2011-09-21 | Charité Universitätsmedizin Berlin | High throughput analysis of T-cell receptor repertoires |
| WO2011139372A1 (en) | 2010-05-06 | 2011-11-10 | Sequenta, Inc. | Sequence analysis of complex amplicons |
| US9234240B2 (en) | 2010-05-07 | 2016-01-12 | The Board Of Trustees Of The Leland Stanford Junior University | Measurement and comparison of immune diversity by high-throughput sequencing |
| US20130123120A1 (en) | 2010-05-18 | 2013-05-16 | Natera, Inc. | Highly Multiplex PCR Methods and Compositions |
| EP2580353B1 (en) | 2010-06-11 | 2015-07-29 | Life Technologies Corporation | Alternative nucleotide flows in sequencing-by-synthesis methods |
| WO2012027503A2 (en) | 2010-08-24 | 2012-03-01 | Fred Hutchinson Cancer Research Center | Method of measuring adaptive immunity |
| ES2523140T3 (es) | 2010-09-21 | 2014-11-21 | Population Genetics Technologies Ltd. | Aumento de la confianza en las identificaciones de alelos con el recuento molecular |
| US9562897B2 (en) | 2010-09-30 | 2017-02-07 | Raindance Technologies, Inc. | Sandwich assays in droplets |
| WO2012048340A2 (en) | 2010-10-08 | 2012-04-12 | President And Fellows Of Harvard College | High-throughput immune sequencing |
| EP2625320B1 (en) | 2010-10-08 | 2019-03-27 | President and Fellows of Harvard College | High-throughput single cell barcoding |
| US8753816B2 (en) | 2010-10-26 | 2014-06-17 | Illumina, Inc. | Sequencing methods |
| EP2635679B1 (en) | 2010-11-05 | 2017-04-19 | Illumina, Inc. | Linking sequence reads using paired code tags |
| US9193997B2 (en) * | 2010-12-15 | 2015-11-24 | The Board Of Trustees Of The Leland Stanford Junior University | Measuring and monitoring of cell clonality |
| DK2652155T3 (en) | 2010-12-16 | 2017-02-13 | Gigagen Inc | Methods for Massive Parallel Analysis of Nucleic Acids in Single Cells |
| WO2012118555A1 (en) | 2010-12-29 | 2012-09-07 | Life Technologies Corporation | Time-warped background signal for sequencing-by-synthesis operations |
| WO2012092455A2 (en) | 2010-12-30 | 2012-07-05 | Life Technologies Corporation | Models for analyzing data from sequencing-by-synthesis operations |
| US8759036B2 (en) | 2011-03-21 | 2014-06-24 | Affymetrix, Inc. | Methods for synthesizing pools of probes |
| EP3907297A1 (en) | 2011-04-15 | 2021-11-10 | The Johns Hopkins University | Safe sequencing system |
| CN103732738A (zh) | 2011-04-28 | 2014-04-16 | 小利兰斯坦福大学托管委员会 | 与样品相关的多核苷酸的鉴定 |
| RS64230B1 (sr) | 2011-05-24 | 2023-06-30 | BioNTech SE | Individualizovane vakcine protiv kancera |
| WO2013033721A1 (en) | 2011-09-02 | 2013-03-07 | Atreca, Inc. | Dna barcodes for multiplexed sequencing |
| US20140356339A1 (en) | 2011-09-09 | 2014-12-04 | Sequenta Inc. | Sequence-based measures of immune response |
| US10385475B2 (en) | 2011-09-12 | 2019-08-20 | Adaptive Biotechnologies Corp. | Random array sequencing of low-complexity libraries |
| US20140256592A1 (en) | 2011-10-11 | 2014-09-11 | Sequenta, Inc. | Determining responsiveness of autoimmune patients to dmard treatment |
| CA2853088C (en) | 2011-10-21 | 2018-03-13 | Adaptive Biotechnologies Corporation | Quantification of adaptive immune cell genomes in a complex mixture of cells |
| WO2013066726A1 (en) | 2011-11-04 | 2013-05-10 | Sequenta, Inc. | T-cell receptor clonotypes shared among ankylosing spondylitis patients |
| US20140336059A1 (en) | 2011-12-05 | 2014-11-13 | Sequenta, Inc. | Clonotypes as biometric specimen tags |
| JP2015501644A (ja) | 2011-12-09 | 2015-01-19 | シーケンタ インコーポレイテッド | 免疫活性化を測定する方法 |
| US9824179B2 (en) | 2011-12-09 | 2017-11-21 | Adaptive Biotechnologies Corp. | Diagnosis of lymphoid malignancies and minimal residual disease detection |
| US9499865B2 (en) | 2011-12-13 | 2016-11-22 | Adaptive Biotechnologies Corp. | Detection and measurement of tissue-infiltrating lymphocytes |
| US20150031553A1 (en) | 2011-12-13 | 2015-01-29 | Sequenta, Inc. | Method of measuring immune activation |
| WO2013096480A2 (en) | 2011-12-20 | 2013-06-27 | Sequenta, Inc. | Monitoring transformation of follicular lymphoma to diffuse large b-cell lymphoma by immune repertoire analysis |
| WO2013112655A1 (en) | 2012-01-24 | 2013-08-01 | Gigagen, Inc. | Method for correction of bias in multiplexed amplification |
| ES2776673T3 (es) | 2012-02-27 | 2020-07-31 | Univ North Carolina Chapel Hill | Métodos y usos para etiquetas moleculares |
| WO2013131074A1 (en) | 2012-03-02 | 2013-09-06 | Diogenix, Inc. | Methods and reagents for evaluating autoimmune disease and determining antibody repertoire |
| US20150038346A1 (en) | 2012-03-05 | 2015-02-05 | Sequenta, Inc. | Monitoring immune responsiveness to cancer vaccination |
| JP6302847B2 (ja) | 2012-03-05 | 2018-03-28 | アダプティヴ バイオテクノロジーズ コーポレーション | 頻度が一致したサブユニットからの、対をなす免疫受容体鎖の決定 |
| WO2013134302A1 (en) | 2012-03-05 | 2013-09-12 | Sequenta, Inc. | Monitoring immune responsiveness to cancer vaccination |
| AU2013246050B2 (en) | 2012-04-13 | 2017-03-16 | Adaptive Biotechnologies Corp. | Detection and quantitation of sample contamination in immune repertoire analysis |
| WO2013158936A1 (en) | 2012-04-20 | 2013-10-24 | Sequenta, Inc | Monitoring immunoglobulin heavy chain evolution in b-cell acute lymphoblastic leukemia |
| PL2831276T3 (pl) | 2012-05-08 | 2016-10-31 | Kompozycje i sposób oznaczania i kalibracji dla odchylenia amplifikacji w reakcjach multipleksowej pcr | |
| US20150247201A1 (en) | 2012-05-31 | 2015-09-03 | Malek Faham | Predicting relapse of chronic lymphocytic leukemia patients treated by allogeneic stem cell transplantation |
| US20130324422A1 (en) | 2012-06-04 | 2013-12-05 | Sequenta, Inc. | Detecting disease-correlated clonotypes from fixed samples |
| CN104520443A (zh) | 2012-06-11 | 2015-04-15 | 赛昆塔公司 | 使用序列标签的序列确定方法 |
| AU2013273987B2 (en) | 2012-06-15 | 2018-08-09 | Adaptive Biotechnologies Corporation | Uniquely tagged rearranged adaptive immune receptor genes in a complex gene set |
| AU2013293240A1 (en) | 2012-07-24 | 2015-03-05 | Adaptive Biotechnologies Corp. | Single cell analysis using sequence tags |
| US20160115532A1 (en) | 2012-08-10 | 2016-04-28 | Sequenta, Inc. | High sensitivity mutation detection using sequence tags |
| GB2521570B (en) | 2012-09-24 | 2021-01-06 | Irepertoire Inc | Multiplex pyrosequencing using non-interfering noise cancelling polynucleotide identification tags |
| WO2014062959A1 (en) | 2012-10-19 | 2014-04-24 | Sequenta, Inc. | Monitoring diffuse large b-cell lymphoma from peripheral blood samples |
| US20150247198A1 (en) | 2012-10-19 | 2015-09-03 | Sequenta, Inc. | Monitoring clonotypes of plasma cell proliferative disorders in peripheral blood |
| AU2013335021A1 (en) | 2012-10-22 | 2015-05-07 | Adaptive Biotechnologies Corp. | Monitoring mantle cell lymphoma clonotypes in peripheral blood after immunotransplant |
| AU2014218910A1 (en) | 2013-02-22 | 2015-08-20 | Adaptive Biotechnologies Corp. | Rare clonotypes and uses thereof |
| US20140255944A1 (en) | 2013-03-08 | 2014-09-11 | Sequenta, Inc. | Monitoring treatment-resistant clones in lymphoid and myeloid neoplasms by relative levels of evolved clonotypes |
| US20140255929A1 (en) | 2013-03-11 | 2014-09-11 | Sequenta, Inc. | Mosaic tags for labeling templates in large-scale amplifications |
| US9708657B2 (en) | 2013-07-01 | 2017-07-18 | Adaptive Biotechnologies Corp. | Method for generating clonotype profiles using sequence tags |
| US20160186260A1 (en) | 2013-07-26 | 2016-06-30 | Sequenta, Llc | Cancer vaccination with antigen evolution |
| US20160258025A1 (en) | 2013-10-18 | 2016-09-08 | The Regents Of The University Of California | Predicting patient responsiveness to immune checkpoint inhibitors |
| US20150218656A1 (en) | 2014-02-03 | 2015-08-06 | Adaptive Biotechnologies Corp. | Methods for detection and diagnosis of a lymphoid malignancy using high throughput sequencing |
| US10066265B2 (en) | 2014-04-01 | 2018-09-04 | Adaptive Biotechnologies Corp. | Determining antigen-specific t-cells |
| US11390921B2 (en) | 2014-04-01 | 2022-07-19 | Adaptive Biotechnologies Corporation | Determining WT-1 specific T cells and WT-1 specific T cell receptors (TCRs) |
| ES2777529T3 (es) | 2014-04-17 | 2020-08-05 | Adaptive Biotechnologies Corp | Cuantificación de genomas de células inmunitarias adaptativas en una mezcla compleja de células |
| CA2966201A1 (en) | 2014-10-29 | 2016-05-06 | Adaptive Biotechnologies Corp. | Highly-multiplexed simultaneous detection of nucleic acids encoding paired adaptive immune receptor heterodimers from many samples |
-
2009
- 2009-11-09 CN CN200980153756.7A patent/CN102272327B/zh active Active
- 2009-11-09 EP EP13195379.6A patent/EP2719774B8/en active Active
- 2009-11-09 EP EP20157266.6A patent/EP3699296A1/en active Pending
- 2009-11-09 CN CN201410350386.9A patent/CN104195227B/zh active Active
- 2009-11-09 ES ES13195379T patent/ES2781754T3/es active Active
- 2009-11-09 GB GB1009641A patent/GB2467704B/en active Active
- 2009-11-09 GB GB1209668.1A patent/GB2488700B/en active Active
- 2009-11-09 EP EP24152841.3A patent/EP4335932A2/en active Pending
- 2009-11-09 WO PCT/US2009/006053 patent/WO2010053587A2/en active Application Filing
- 2009-11-09 GB GB1300533.5A patent/GB2497007B/en active Active
- 2009-11-09 ES ES09764927.1T patent/ES2453066T3/es active Active
- 2009-11-09 SG SG2013082532A patent/SG195652A1/en unknown
- 2009-11-09 US US12/615,263 patent/US8236503B2/en active Active
- 2009-11-09 EP EP09764927.1A patent/EP2364368B1/en not_active Revoked
- 2009-11-09 GB GB1105068.9A patent/GB2477439B/en active Active
- 2009-11-09 AU AU2009311588A patent/AU2009311588B2/en active Active
- 2009-11-09 JP JP2011535569A patent/JP5798926B2/ja active Active
- 2009-11-09 CA CA2742380A patent/CA2742380C/en active Active
- 2009-11-09 GB GB1120209.0A patent/GB2483810B/en active Active
-
2011
- 2011-05-04 US US13/100,395 patent/US8507205B2/en active Active
- 2011-08-19 US US13/214,111 patent/US20120135409A1/en active Granted
-
2012
- 2012-04-30 US US13/459,701 patent/US9217176B2/en active Active
- 2012-05-10 US US13/468,323 patent/US8795970B2/en active Active
-
2013
- 2013-05-30 US US13/905,406 patent/US20130344066A1/en not_active Abandoned
- 2013-06-03 US US13/908,813 patent/US9347099B2/en active Active
-
2014
- 2014-07-11 US US14/329,873 patent/US9228232B2/en active Active
-
2015
- 2015-08-24 JP JP2015164457A patent/JP6112577B2/ja active Active
-
2016
- 2016-01-04 US US14/987,165 patent/US10266901B2/en active Active
- 2016-04-20 US US15/133,932 patent/US20160230236A1/en not_active Abandoned
-
2017
- 2017-11-22 US US15/820,655 patent/US10246752B2/en active Active
- 2017-11-30 US US15/827,759 patent/US10760133B2/en active Active
-
2018
- 2018-09-05 US US16/121,995 patent/US10865453B2/en active Active
- 2018-12-13 US US16/218,535 patent/US11021757B2/en active Active
- 2018-12-17 US US16/222,052 patent/US11001895B2/en active Active
-
2021
- 2021-04-16 US US17/232,961 patent/US20210310076A1/en active Pending
Also Published As
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| JP6112577B2 (ja) | 配列解析によって病態をモニターする方法 | |
| JP6246971B2 (ja) | クロノタイププロファイルを用いた健康状態および疾患状態のモニタリング | |
| US20170349954A1 (en) | Monitoring health and disease status using clonotype profiles | |
| US20110207134A1 (en) | Monitoring health and disease status using clonotype profiles |
Legal Events
| Date | Code | Title | Description |
|---|---|---|---|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20121031 |
|
| A621 | Written request for application examination |
Free format text: JAPANESE INTERMEDIATE CODE: A621 Effective date: 20121031 |
|
| A131 | Notification of reasons for refusal |
Free format text: JAPANESE INTERMEDIATE CODE: A131 Effective date: 20140428 |
|
| A601 | Written request for extension of time |
Free format text: JAPANESE INTERMEDIATE CODE: A601 Effective date: 20140725 |
|
| A602 | Written permission of extension of time |
Free format text: JAPANESE INTERMEDIATE CODE: A602 Effective date: 20140801 |
|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20141017 |
|
| A131 | Notification of reasons for refusal |
Free format text: JAPANESE INTERMEDIATE CODE: A131 Effective date: 20150319 |
|
| A601 | Written request for extension of time |
Free format text: JAPANESE INTERMEDIATE CODE: A601 Effective date: 20150619 |
|
| RD04 | Notification of resignation of power of attorney |
Free format text: JAPANESE INTERMEDIATE CODE: A7424 Effective date: 20150622 |
|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20150626 |
|
| TRDD | Decision of grant or rejection written | ||
| A01 | Written decision to grant a patent or to grant a registration (utility model) |
Free format text: JAPANESE INTERMEDIATE CODE: A01 Effective date: 20150723 |
|
| A61 | First payment of annual fees (during grant procedure) |
Free format text: JAPANESE INTERMEDIATE CODE: A61 Effective date: 20150824 |
|
| R150 | Certificate of patent or registration of utility model |
Ref document number: 5798926 Country of ref document: JP Free format text: JAPANESE INTERMEDIATE CODE: R150 |
|
| S111 | Request for change of ownership or part of ownership |
Free format text: JAPANESE INTERMEDIATE CODE: R313111 |
|
| R350 | Written notification of registration of transfer |
Free format text: JAPANESE INTERMEDIATE CODE: R350 |
|
| S111 | Request for change of ownership or part of ownership |
Free format text: JAPANESE INTERMEDIATE CODE: R313113 |
|
| R350 | Written notification of registration of transfer |
Free format text: JAPANESE INTERMEDIATE CODE: R350 |
|
| R250 | Receipt of annual fees |
Free format text: JAPANESE INTERMEDIATE CODE: R250 |
|
| R250 | Receipt of annual fees |
Free format text: JAPANESE INTERMEDIATE CODE: R250 |
|
| R250 | Receipt of annual fees |
Free format text: JAPANESE INTERMEDIATE CODE: R250 |
|
| R250 | Receipt of annual fees |
Free format text: JAPANESE INTERMEDIATE CODE: R250 |
|
| R250 | Receipt of annual fees |
Free format text: JAPANESE INTERMEDIATE CODE: R250 |
|
| R250 | Receipt of annual fees |
Free format text: JAPANESE INTERMEDIATE CODE: R250 |