DE69839242T2 - Rrekombinante proteine eines pakistani-stammes von hepatitis-e-virus, ihre verwendung in diagnotischen verfahren und als impfstoff - Google Patents
Rrekombinante proteine eines pakistani-stammes von hepatitis-e-virus, ihre verwendung in diagnotischen verfahren und als impfstoff Download PDFInfo
- Publication number
- DE69839242T2 DE69839242T2 DE69839242T DE69839242T DE69839242T2 DE 69839242 T2 DE69839242 T2 DE 69839242T2 DE 69839242 T DE69839242 T DE 69839242T DE 69839242 T DE69839242 T DE 69839242T DE 69839242 T2 DE69839242 T2 DE 69839242T2
- Authority
- DE
- Germany
- Prior art keywords
- protein
- hev
- hepatitis
- virus
- open reading
- Prior art date
- Legal status (The legal status is an assumption and is not a legal conclusion. Google has not performed a legal analysis and makes no representation as to the accuracy of the status listed.)
- Expired - Lifetime
Links
- 241000724675 Hepatitis E virus Species 0.000 title claims abstract description 358
- 108090000623 proteins and genes Proteins 0.000 title claims abstract description 315
- 102000004169 proteins and genes Human genes 0.000 title claims abstract description 292
- 229960005486 vaccine Drugs 0.000 title claims abstract description 42
- 238000002405 diagnostic procedure Methods 0.000 title description 4
- 208000015181 infectious disease Diseases 0.000 claims abstract description 74
- 108700026244 Open Reading Frames Proteins 0.000 claims abstract description 59
- 201000010284 hepatitis E Diseases 0.000 claims abstract description 36
- 230000014509 gene expression Effects 0.000 claims abstract description 35
- 210000004027 cell Anatomy 0.000 claims description 114
- 150000001413 amino acids Chemical class 0.000 claims description 82
- 238000000034 method Methods 0.000 claims description 54
- 238000001514 detection method Methods 0.000 claims description 25
- 230000003053 immunization Effects 0.000 claims description 24
- FWMNVWWHGCHHJJ-SKKKGAJSSA-N 4-amino-1-[(2r)-6-amino-2-[[(2r)-2-[[(2r)-2-[[(2r)-2-amino-3-phenylpropanoyl]amino]-3-phenylpropanoyl]amino]-4-methylpentanoyl]amino]hexanoyl]piperidine-4-carboxylic acid Chemical compound C([C@H](C(=O)N[C@H](CC(C)C)C(=O)N[C@H](CCCCN)C(=O)N1CCC(N)(CC1)C(O)=O)NC(=O)[C@H](N)CC=1C=CC=CC=1)C1=CC=CC=C1 FWMNVWWHGCHHJJ-SKKKGAJSSA-N 0.000 claims description 22
- 108020004414 DNA Proteins 0.000 claims description 21
- 210000004899 c-terminal region Anatomy 0.000 claims description 20
- 238000004519 manufacturing process Methods 0.000 claims description 19
- 239000002773 nucleotide Substances 0.000 claims description 19
- 125000003729 nucleotide group Chemical group 0.000 claims description 19
- 108700006290 Hepatitis E virus ORF2 Proteins 0.000 claims description 18
- 239000013604 expression vector Substances 0.000 claims description 16
- 125000002924 primary amino group Chemical group [H]N([H])* 0.000 claims description 14
- 241000124008 Mammalia Species 0.000 claims description 13
- 102000053602 DNA Human genes 0.000 claims description 9
- 239000000523 sample Substances 0.000 claims description 9
- 239000012472 biological sample Substances 0.000 claims description 7
- 239000008194 pharmaceutical composition Substances 0.000 claims description 7
- 230000008569 process Effects 0.000 claims description 5
- 238000003259 recombinant expression Methods 0.000 claims description 5
- 239000003085 diluting agent Substances 0.000 claims description 4
- 239000003814 drug Substances 0.000 claims description 4
- 239000003937 drug carrier Substances 0.000 claims description 3
- 239000000546 pharmaceutical excipient Substances 0.000 claims description 3
- 230000002265 prevention Effects 0.000 claims description 3
- 239000000427 antigen Substances 0.000 abstract description 103
- 108091007433 antigens Proteins 0.000 abstract description 102
- 102000036639 antigens Human genes 0.000 abstract description 102
- 230000002163 immunogen Effects 0.000 abstract description 30
- 238000003018 immunoassay Methods 0.000 abstract description 16
- 235000018102 proteins Nutrition 0.000 description 250
- 241001465754 Metazoa Species 0.000 description 142
- 238000002965 ELISA Methods 0.000 description 62
- 235000001014 amino acid Nutrition 0.000 description 54
- 208000006454 hepatitis Diseases 0.000 description 54
- 231100000283 hepatitis Toxicity 0.000 description 54
- 210000002966 serum Anatomy 0.000 description 54
- 229940024606 amino acid Drugs 0.000 description 53
- 108010082126 Alanine transaminase Proteins 0.000 description 52
- 241000700605 Viruses Species 0.000 description 52
- 102100036475 Alanine aminotransferase 1 Human genes 0.000 description 51
- 239000012634 fragment Substances 0.000 description 48
- 241000238631 Hexapoda Species 0.000 description 47
- 101710159752 Poly(3-hydroxyalkanoate) polymerase subunit PhaE Proteins 0.000 description 41
- 101710130262 Probable Vpr-like protein Proteins 0.000 description 41
- FAPWRFPIFSIZLT-UHFFFAOYSA-M Sodium chloride Chemical compound [Na+].[Cl-] FAPWRFPIFSIZLT-UHFFFAOYSA-M 0.000 description 39
- 239000013598 vector Substances 0.000 description 39
- 241000701447 unidentified baculovirus Species 0.000 description 36
- 241000282567 Macaca fascicularis Species 0.000 description 33
- 238000010790 dilution Methods 0.000 description 33
- 239000012895 dilution Substances 0.000 description 33
- 241000282693 Cercopithecidae Species 0.000 description 32
- 210000003608 fece Anatomy 0.000 description 30
- 150000007523 nucleic acids Chemical group 0.000 description 30
- 108091028043 Nucleic acid sequence Proteins 0.000 description 29
- 238000011081 inoculation Methods 0.000 description 29
- 239000000203 mixture Substances 0.000 description 28
- 239000000725 suspension Substances 0.000 description 28
- 206010058874 Viraemia Diseases 0.000 description 27
- 239000006228 supernatant Substances 0.000 description 27
- 239000013592 cell lysate Substances 0.000 description 26
- 238000004458 analytical method Methods 0.000 description 23
- 230000000694 effects Effects 0.000 description 23
- 230000002550 fecal effect Effects 0.000 description 22
- 238000002649 immunization Methods 0.000 description 22
- 239000002245 particle Substances 0.000 description 22
- 125000003275 alpha amino acid group Chemical group 0.000 description 21
- 238000001262 western blot Methods 0.000 description 21
- 239000013615 primer Substances 0.000 description 20
- 239000011780 sodium chloride Substances 0.000 description 20
- LFQSCWFLJHTTHZ-UHFFFAOYSA-N Ethanol Chemical compound CCO LFQSCWFLJHTTHZ-UHFFFAOYSA-N 0.000 description 18
- 241000288906 Primates Species 0.000 description 18
- 239000000902 placebo Substances 0.000 description 18
- 239000000047 product Substances 0.000 description 18
- 230000003612 virological effect Effects 0.000 description 18
- 238000010240 RT-PCR analysis Methods 0.000 description 17
- 108010008281 Recombinant Fusion Proteins Proteins 0.000 description 17
- 102000007056 Recombinant Fusion Proteins Human genes 0.000 description 17
- 229940068196 placebo Drugs 0.000 description 17
- 108090000765 processed proteins & peptides Proteins 0.000 description 17
- QKNYBSVHEMOAJP-UHFFFAOYSA-N 2-amino-2-(hydroxymethyl)propane-1,3-diol;hydron;chloride Chemical compound Cl.OCC(N)(CO)CO QKNYBSVHEMOAJP-UHFFFAOYSA-N 0.000 description 16
- 239000012160 loading buffer Substances 0.000 description 16
- 101710167800 Capsid assembly scaffolding protein Proteins 0.000 description 14
- 101710113540 ORF2 protein Proteins 0.000 description 14
- 101710090523 Putative movement protein Proteins 0.000 description 14
- 239000000499 gel Substances 0.000 description 14
- 241000282579 Pan Species 0.000 description 13
- 238000003556 assay Methods 0.000 description 13
- 230000004927 fusion Effects 0.000 description 13
- HEDRZPFGACZZDS-UHFFFAOYSA-N Chloroform Chemical compound ClC(Cl)Cl HEDRZPFGACZZDS-UHFFFAOYSA-N 0.000 description 12
- 241000588724 Escherichia coli Species 0.000 description 12
- 102000005720 Glutathione transferase Human genes 0.000 description 12
- 108010070675 Glutathione transferase Proteins 0.000 description 12
- 239000006166 lysate Substances 0.000 description 12
- 239000002299 complementary DNA Substances 0.000 description 11
- 230000029142 excretion Effects 0.000 description 11
- 210000002381 plasma Anatomy 0.000 description 11
- 238000012360 testing method Methods 0.000 description 11
- 241000282560 Macaca mulatta Species 0.000 description 10
- 208000037265 diseases, disorders, signs and symptoms Diseases 0.000 description 10
- 238000009472 formulation Methods 0.000 description 10
- 238000002523 gelfiltration Methods 0.000 description 10
- 238000001990 intravenous administration Methods 0.000 description 10
- 108020004707 nucleic acids Proteins 0.000 description 10
- 102000039446 nucleic acids Human genes 0.000 description 10
- 102000004196 processed proteins & peptides Human genes 0.000 description 10
- PEDCQBHIVMGVHV-UHFFFAOYSA-N Glycerine Chemical compound OCC(O)CO PEDCQBHIVMGVHV-UHFFFAOYSA-N 0.000 description 9
- KFZMGEQAYNKOFK-UHFFFAOYSA-N Isopropanol Chemical compound CC(C)O KFZMGEQAYNKOFK-UHFFFAOYSA-N 0.000 description 9
- KDXKERNSBIXSRK-UHFFFAOYSA-N Lysine Natural products NCCCCC(N)C(O)=O KDXKERNSBIXSRK-UHFFFAOYSA-N 0.000 description 9
- 240000004808 Saccharomyces cerevisiae Species 0.000 description 9
- 235000014680 Saccharomyces cerevisiae Nutrition 0.000 description 9
- 239000000872 buffer Substances 0.000 description 9
- 201000010099 disease Diseases 0.000 description 9
- 239000013612 plasmid Substances 0.000 description 9
- 108091032973 (ribonucleotides)n+m Proteins 0.000 description 8
- 108091003079 Bovine Serum Albumin Proteins 0.000 description 8
- DBMJMQXJHONAFJ-UHFFFAOYSA-M Sodium laurylsulphate Chemical compound [Na+].CCCCCCCCCCCCOS([O-])(=O)=O DBMJMQXJHONAFJ-UHFFFAOYSA-M 0.000 description 8
- 210000004369 blood Anatomy 0.000 description 8
- 239000008280 blood Substances 0.000 description 8
- AIYUHDOJVYHVIT-UHFFFAOYSA-M caesium chloride Chemical compound [Cl-].[Cs+] AIYUHDOJVYHVIT-UHFFFAOYSA-M 0.000 description 8
- 238000004587 chromatography analysis Methods 0.000 description 8
- 230000003247 decreasing effect Effects 0.000 description 8
- 238000002360 preparation method Methods 0.000 description 8
- 238000002255 vaccination Methods 0.000 description 8
- 230000009385 viral infection Effects 0.000 description 8
- 241000283707 Capra Species 0.000 description 7
- 101710172711 Structural protein Proteins 0.000 description 7
- 101800003447 VP53 Proteins 0.000 description 7
- 238000005349 anion exchange Methods 0.000 description 7
- 230000000890 antigenic effect Effects 0.000 description 7
- 238000010367 cloning Methods 0.000 description 7
- 239000012528 membrane Substances 0.000 description 7
- 238000000746 purification Methods 0.000 description 7
- 230000002829 reductive effect Effects 0.000 description 7
- 238000000108 ultra-filtration Methods 0.000 description 7
- QFVHZQCOUORWEI-UHFFFAOYSA-N 4-[(4-anilino-5-sulfonaphthalen-1-yl)diazenyl]-5-hydroxynaphthalene-2,7-disulfonic acid Chemical compound C=12C(O)=CC(S(O)(=O)=O)=CC2=CC(S(O)(=O)=O)=CC=1N=NC(C1=CC=CC(=C11)S(O)(=O)=O)=CC=C1NC1=CC=CC=C1 QFVHZQCOUORWEI-UHFFFAOYSA-N 0.000 description 6
- 108091034117 Oligonucleotide Proteins 0.000 description 6
- 241000282577 Pan troglodytes Species 0.000 description 6
- 239000012506 Sephacryl® Substances 0.000 description 6
- 238000012300 Sequence Analysis Methods 0.000 description 6
- 230000027455 binding Effects 0.000 description 6
- 239000003153 chemical reaction reagent Substances 0.000 description 6
- 238000005516 engineering process Methods 0.000 description 6
- 210000003527 eukaryotic cell Anatomy 0.000 description 6
- 238000002474 experimental method Methods 0.000 description 6
- 230000002458 infectious effect Effects 0.000 description 6
- 238000004949 mass spectrometry Methods 0.000 description 6
- 239000000463 material Substances 0.000 description 6
- 239000002953 phosphate buffered saline Substances 0.000 description 6
- 230000004044 response Effects 0.000 description 6
- 230000002441 reversible effect Effects 0.000 description 6
- 239000000243 solution Substances 0.000 description 6
- 238000007619 statistical method Methods 0.000 description 6
- 238000012546 transfer Methods 0.000 description 6
- 101000787132 Acidithiobacillus ferridurans Uncharacterized 8.2 kDa protein in mobL 3'region Proteins 0.000 description 5
- 101000827262 Acidithiobacillus ferrooxidans Uncharacterized 18.9 kDa protein in mobE 3'region Proteins 0.000 description 5
- 101000811747 Antithamnion sp. UPF0051 protein in atpA 3'region Proteins 0.000 description 5
- 101000827607 Bacillus phage SPP1 Uncharacterized 8.5 kDa protein in GP2-GP6 intergenic region Proteins 0.000 description 5
- 101000961975 Bacillus thuringiensis Uncharacterized 13.4 kDa protein Proteins 0.000 description 5
- 241000894006 Bacteria Species 0.000 description 5
- 101000964407 Caldicellulosiruptor saccharolyticus Uncharacterized 10.7 kDa protein in xynB 3'region Proteins 0.000 description 5
- 101000768777 Haloferax lucentense (strain DSM 14919 / JCM 9276 / NCIMB 13854 / Aa 2.2) Uncharacterized 50.6 kDa protein in the 5'region of gyrA and gyrB Proteins 0.000 description 5
- 206010019799 Hepatitis viral Diseases 0.000 description 5
- 241000282412 Homo Species 0.000 description 5
- 108060003951 Immunoglobulin Proteins 0.000 description 5
- 101000607404 Infectious laryngotracheitis virus (strain Thorne V882) Protein UL24 homolog Proteins 0.000 description 5
- 101000735632 Klebsiella pneumoniae Uncharacterized 8.8 kDa protein in aacA4 3'region Proteins 0.000 description 5
- 239000012564 Q sepharose fast flow resin Substances 0.000 description 5
- 101000818100 Spirochaeta aurantia Uncharacterized 12.7 kDa protein in trpE 5'region Proteins 0.000 description 5
- 101001037658 Streptomyces coelicolor (strain ATCC BAA-471 / A3(2) / M145) Glucokinase Proteins 0.000 description 5
- 101001120268 Streptomyces griseus Protein Y Proteins 0.000 description 5
- 208000036142 Viral infection Diseases 0.000 description 5
- 229940037003 alum Drugs 0.000 description 5
- 230000003321 amplification Effects 0.000 description 5
- 239000007864 aqueous solution Substances 0.000 description 5
- 230000001580 bacterial effect Effects 0.000 description 5
- 102000037865 fusion proteins Human genes 0.000 description 5
- 108020001507 fusion proteins Proteins 0.000 description 5
- 239000007789 gas Substances 0.000 description 5
- 102000018358 immunoglobulin Human genes 0.000 description 5
- 238000011534 incubation Methods 0.000 description 5
- 208000019423 liver disease Diseases 0.000 description 5
- 238000011068 loading method Methods 0.000 description 5
- 210000004698 lymphocyte Anatomy 0.000 description 5
- 238000003199 nucleic acid amplification method Methods 0.000 description 5
- 239000012071 phase Substances 0.000 description 5
- QKFJKGMPGYROCL-UHFFFAOYSA-N phenyl isothiocyanate Chemical compound S=C=NC1=CC=CC=C1 QKFJKGMPGYROCL-UHFFFAOYSA-N 0.000 description 5
- 229920002401 polyacrylamide Polymers 0.000 description 5
- 239000002244 precipitate Substances 0.000 description 5
- 238000009589 serological test Methods 0.000 description 5
- 239000007787 solid Substances 0.000 description 5
- 241000894007 species Species 0.000 description 5
- 239000003381 stabilizer Substances 0.000 description 5
- 239000011550 stock solution Substances 0.000 description 5
- 230000001225 therapeutic effect Effects 0.000 description 5
- 201000001862 viral hepatitis Diseases 0.000 description 5
- XLYOFNOQVPJJNP-UHFFFAOYSA-N water Substances O XLYOFNOQVPJJNP-UHFFFAOYSA-N 0.000 description 5
- 241000867607 Chlorocebus sabaeus Species 0.000 description 4
- 238000011537 Coomassie blue staining Methods 0.000 description 4
- 102000004190 Enzymes Human genes 0.000 description 4
- 108090000790 Enzymes Proteins 0.000 description 4
- DHMQDGOQFOQNFH-UHFFFAOYSA-N Glycine Chemical compound NCC(O)=O DHMQDGOQFOQNFH-UHFFFAOYSA-N 0.000 description 4
- 239000000020 Nitrocellulose Substances 0.000 description 4
- ISWSIDIOOBJBQZ-UHFFFAOYSA-N Phenol Chemical compound OC1=CC=CC=C1 ISWSIDIOOBJBQZ-UHFFFAOYSA-N 0.000 description 4
- 241000288961 Saguinus imperator Species 0.000 description 4
- 241000282695 Saimiri Species 0.000 description 4
- 229920002684 Sepharose Polymers 0.000 description 4
- JLCPHMBAVCMARE-UHFFFAOYSA-N [3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-[[3-[[3-[[3-[[3-[[3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-hydroxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methyl [5-(6-aminopurin-9-yl)-2-(hydroxymethyl)oxolan-3-yl] hydrogen phosphate Polymers Cc1cn(C2CC(OP(O)(=O)OCC3OC(CC3OP(O)(=O)OCC3OC(CC3O)n3cnc4c3nc(N)[nH]c4=O)n3cnc4c3nc(N)[nH]c4=O)C(COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3CO)n3cnc4c(N)ncnc34)n3ccc(N)nc3=O)n3cnc4c(N)ncnc34)n3ccc(N)nc3=O)n3ccc(N)nc3=O)n3ccc(N)nc3=O)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cc(C)c(=O)[nH]c3=O)n3cc(C)c(=O)[nH]c3=O)n3ccc(N)nc3=O)n3cc(C)c(=O)[nH]c3=O)n3cnc4c3nc(N)[nH]c4=O)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)O2)c(=O)[nH]c1=O JLCPHMBAVCMARE-UHFFFAOYSA-N 0.000 description 4
- 239000011543 agarose gel Substances 0.000 description 4
- 230000003302 anti-idiotype Effects 0.000 description 4
- 230000002155 anti-virotic effect Effects 0.000 description 4
- 230000005875 antibody response Effects 0.000 description 4
- 239000003443 antiviral agent Substances 0.000 description 4
- 230000015572 biosynthetic process Effects 0.000 description 4
- 229940098773 bovine serum albumin Drugs 0.000 description 4
- 125000003178 carboxy group Chemical group [H]OC(*)=O 0.000 description 4
- 238000005119 centrifugation Methods 0.000 description 4
- 238000003776 cleavage reaction Methods 0.000 description 4
- 238000012217 deletion Methods 0.000 description 4
- 230000037430 deletion Effects 0.000 description 4
- VHJLVAABSRFDPM-QWWZWVQMSA-N dithiothreitol Chemical compound SC[C@@H](O)[C@H](O)CS VHJLVAABSRFDPM-QWWZWVQMSA-N 0.000 description 4
- 238000010828 elution Methods 0.000 description 4
- 210000004408 hybridoma Anatomy 0.000 description 4
- 230000000521 hyperimmunizing effect Effects 0.000 description 4
- 238000001727 in vivo Methods 0.000 description 4
- 238000002347 injection Methods 0.000 description 4
- 239000007924 injection Substances 0.000 description 4
- 239000002054 inoculum Substances 0.000 description 4
- 108020004999 messenger RNA Proteins 0.000 description 4
- 229920001220 nitrocellulos Polymers 0.000 description 4
- 229920001184 polypeptide Polymers 0.000 description 4
- 238000001556 precipitation Methods 0.000 description 4
- 230000000069 prophylactic effect Effects 0.000 description 4
- 238000001742 protein purification Methods 0.000 description 4
- 230000007017 scission Effects 0.000 description 4
- 238000006467 substitution reaction Methods 0.000 description 4
- 238000003786 synthesis reaction Methods 0.000 description 4
- 239000003643 water by type Substances 0.000 description 4
- 230000003442 weekly effect Effects 0.000 description 4
- WEVYAHXRMPXWCK-UHFFFAOYSA-N Acetonitrile Chemical compound CC#N WEVYAHXRMPXWCK-UHFFFAOYSA-N 0.000 description 3
- 102000002260 Alkaline Phosphatase Human genes 0.000 description 3
- 108020004774 Alkaline Phosphatase Proteins 0.000 description 3
- 241000282708 Aotus <primate> Species 0.000 description 3
- 101000666833 Autographa californica nuclear polyhedrosis virus Uncharacterized 20.8 kDa protein in FGF-VUBI intergenic region Proteins 0.000 description 3
- 101000977027 Azospirillum brasilense Uncharacterized protein in nodG 5'region Proteins 0.000 description 3
- 101000933555 Bacillus subtilis (strain 168) Biofilm-surface layer protein A Proteins 0.000 description 3
- 101000962005 Bacillus thuringiensis Uncharacterized 23.6 kDa protein Proteins 0.000 description 3
- 125000001433 C-terminal amino-acid group Chemical group 0.000 description 3
- 102000012286 Chitinases Human genes 0.000 description 3
- 108010022172 Chitinases Proteins 0.000 description 3
- 101000785191 Drosophila melanogaster Uncharacterized 50 kDa protein in type I retrotransposable element R1DM Proteins 0.000 description 3
- KCXVZYZYPLLWCC-UHFFFAOYSA-N EDTA Chemical compound OC(=O)CN(CC(O)=O)CCN(CC(O)=O)CC(O)=O KCXVZYZYPLLWCC-UHFFFAOYSA-N 0.000 description 3
- 101000747704 Enterobacteria phage N4 Uncharacterized protein Gp1 Proteins 0.000 description 3
- 101000861206 Enterococcus faecalis (strain ATCC 700802 / V583) Uncharacterized protein EF_A0048 Proteins 0.000 description 3
- 101000769180 Escherichia coli Uncharacterized 11.1 kDa protein Proteins 0.000 description 3
- 108010010803 Gelatin Proteins 0.000 description 3
- 102100034343 Integrase Human genes 0.000 description 3
- ROHFNLRQFUQHCH-YFKPBYRVSA-N L-leucine Chemical compound CC(C)C[C@H](N)C(O)=O ROHFNLRQFUQHCH-YFKPBYRVSA-N 0.000 description 3
- 101000976301 Leptospira interrogans Uncharacterized 35 kDa protein in sph 3'region Proteins 0.000 description 3
- ROHFNLRQFUQHCH-UHFFFAOYSA-N Leucine Natural products CC(C)CC(N)C(O)=O ROHFNLRQFUQHCH-UHFFFAOYSA-N 0.000 description 3
- 241000282561 Macaca nemestrina Species 0.000 description 3
- 101000658690 Neisseria meningitidis serogroup B Transposase for insertion sequence element IS1106 Proteins 0.000 description 3
- 101000748660 Pseudomonas savastanoi Uncharacterized 21 kDa protein in iaaL 5'region Proteins 0.000 description 3
- 238000002123 RNA extraction Methods 0.000 description 3
- 108010092799 RNA-directed DNA polymerase Proteins 0.000 description 3
- 101000584469 Rice tungro bacilliform virus (isolate Philippines) Protein P1 Proteins 0.000 description 3
- 101000773449 Sinorhizobium fredii (strain NBRC 101917 / NGR234) Uncharacterized HTH-type transcriptional regulator y4sM Proteins 0.000 description 3
- 101000818096 Spirochaeta aurantia Uncharacterized 15.5 kDa protein in trpE 3'region Proteins 0.000 description 3
- 101000766081 Streptomyces ambofaciens Uncharacterized HTH-type transcriptional regulator in unstable DNA locus Proteins 0.000 description 3
- 101000987243 Streptomyces griseus Probable cadicidin biosynthesis thioesterase Proteins 0.000 description 3
- 101000804403 Synechococcus elongatus (strain PCC 7942 / FACHB-805) Uncharacterized HIT-like protein Synpcc7942_1390 Proteins 0.000 description 3
- 101000750910 Synechococcus elongatus (strain PCC 7942 / FACHB-805) Uncharacterized HTH-type transcriptional regulator Synpcc7942_2319 Proteins 0.000 description 3
- 101000644897 Synechococcus sp. (strain ATCC 27264 / PCC 7002 / PR-6) Uncharacterized protein SYNPCC7002_B0001 Proteins 0.000 description 3
- 108020000999 Viral RNA Proteins 0.000 description 3
- 101000916336 Xenopus laevis Transposon TX1 uncharacterized 82 kDa protein Proteins 0.000 description 3
- 101001000760 Zea mays Putative Pol polyprotein from transposon element Bs1 Proteins 0.000 description 3
- 101000678262 Zymomonas mobilis subsp. mobilis (strain ATCC 10988 / DSM 424 / LMG 404 / NCIMB 8938 / NRRL B-806 / ZM1) 65 kDa protein Proteins 0.000 description 3
- 238000003277 amino acid sequence analysis Methods 0.000 description 3
- 238000005571 anion exchange chromatography Methods 0.000 description 3
- 230000000692 anti-sense effect Effects 0.000 description 3
- 230000008901 benefit Effects 0.000 description 3
- 230000000903 blocking effect Effects 0.000 description 3
- 239000000969 carrier Substances 0.000 description 3
- 238000004113 cell culture Methods 0.000 description 3
- 229920002678 cellulose Polymers 0.000 description 3
- 239000001913 cellulose Substances 0.000 description 3
- 235000010980 cellulose Nutrition 0.000 description 3
- 238000006243 chemical reaction Methods 0.000 description 3
- 238000004140 cleaning Methods 0.000 description 3
- 230000000295 complement effect Effects 0.000 description 3
- 238000010276 construction Methods 0.000 description 3
- 238000012258 culturing Methods 0.000 description 3
- 238000003745 diagnosis Methods 0.000 description 3
- 230000029087 digestion Effects 0.000 description 3
- 238000000605 extraction Methods 0.000 description 3
- 239000012894 fetal calf serum Substances 0.000 description 3
- 239000008273 gelatin Substances 0.000 description 3
- 229920000159 gelatin Polymers 0.000 description 3
- 235000019322 gelatine Nutrition 0.000 description 3
- 235000011852 gelatine desserts Nutrition 0.000 description 3
- 235000011187 glycerol Nutrition 0.000 description 3
- 230000013595 glycosylation Effects 0.000 description 3
- 238000006206 glycosylation reaction Methods 0.000 description 3
- 208000002672 hepatitis B Diseases 0.000 description 3
- 230000007062 hydrolysis Effects 0.000 description 3
- 238000006460 hydrolysis reaction Methods 0.000 description 3
- 238000007918 intramuscular administration Methods 0.000 description 3
- 230000000670 limiting effect Effects 0.000 description 3
- 210000004185 liver Anatomy 0.000 description 3
- 239000003550 marker Substances 0.000 description 3
- 239000003094 microcapsule Substances 0.000 description 3
- 230000003287 optical effect Effects 0.000 description 3
- 102000013415 peroxidase activity proteins Human genes 0.000 description 3
- 108040007629 peroxidase activity proteins Proteins 0.000 description 3
- 229940117953 phenylisothiocyanate Drugs 0.000 description 3
- 108091033319 polynucleotide Proteins 0.000 description 3
- 238000012545 processing Methods 0.000 description 3
- 230000001681 protective effect Effects 0.000 description 3
- 230000009467 reduction Effects 0.000 description 3
- 108091008146 restriction endonucleases Proteins 0.000 description 3
- 238000010839 reverse transcription Methods 0.000 description 3
- 238000012552 review Methods 0.000 description 3
- 230000028327 secretion Effects 0.000 description 3
- 238000012163 sequencing technique Methods 0.000 description 3
- 230000000405 serological effect Effects 0.000 description 3
- 239000012679 serum free medium Substances 0.000 description 3
- 239000007790 solid phase Substances 0.000 description 3
- 239000007921 spray Substances 0.000 description 3
- 238000010186 staining Methods 0.000 description 3
- 238000010561 standard procedure Methods 0.000 description 3
- 238000004114 suspension culture Methods 0.000 description 3
- 230000002123 temporal effect Effects 0.000 description 3
- 238000013518 transcription Methods 0.000 description 3
- 230000035897 transcription Effects 0.000 description 3
- 230000014616 translation Effects 0.000 description 3
- 238000011282 treatment Methods 0.000 description 3
- MTCFGRXMJLQNBG-REOHCLBHSA-N (2S)-2-Amino-3-hydroxypropansäure Chemical compound OC[C@H](N)C(O)=O MTCFGRXMJLQNBG-REOHCLBHSA-N 0.000 description 2
- BFSVOASYOCHEOV-UHFFFAOYSA-N 2-diethylaminoethanol Chemical compound CCN(CC)CCO BFSVOASYOCHEOV-UHFFFAOYSA-N 0.000 description 2
- QRXMUCSWCMTJGU-UHFFFAOYSA-N 5-bromo-4-chloro-3-indolyl phosphate Chemical compound C1=C(Br)C(Cl)=C2C(OP(O)(=O)O)=CNC2=C1 QRXMUCSWCMTJGU-UHFFFAOYSA-N 0.000 description 2
- USFZMSVCRYTOJT-UHFFFAOYSA-N Ammonium acetate Chemical compound N.CC(O)=O USFZMSVCRYTOJT-UHFFFAOYSA-N 0.000 description 2
- 239000005695 Ammonium acetate Substances 0.000 description 2
- 239000004475 Arginine Substances 0.000 description 2
- XKRFYHLGVUSROY-UHFFFAOYSA-N Argon Chemical compound [Ar] XKRFYHLGVUSROY-UHFFFAOYSA-N 0.000 description 2
- IJGRMHOSHXDMSA-UHFFFAOYSA-N Atomic nitrogen Chemical compound N#N IJGRMHOSHXDMSA-UHFFFAOYSA-N 0.000 description 2
- BVKZGUZCCUSVTD-UHFFFAOYSA-L Carbonate Chemical compound [O-]C([O-])=O BVKZGUZCCUSVTD-UHFFFAOYSA-L 0.000 description 2
- 229920002134 Carboxymethyl cellulose Polymers 0.000 description 2
- 102000005572 Cathepsin A Human genes 0.000 description 2
- 108010059081 Cathepsin A Proteins 0.000 description 2
- 108020004705 Codon Proteins 0.000 description 2
- 229920002271 DEAE-Sepharose Polymers 0.000 description 2
- 108010067770 Endopeptidase K Proteins 0.000 description 2
- 108020004206 Gamma-glutamyltransferase Proteins 0.000 description 2
- WHUUTDBJXJRKMK-UHFFFAOYSA-N Glutamic acid Natural products OC(=O)C(N)CCC(O)=O WHUUTDBJXJRKMK-UHFFFAOYSA-N 0.000 description 2
- 239000004471 Glycine Substances 0.000 description 2
- 241000701044 Human gammaherpesvirus 4 Species 0.000 description 2
- 206010065042 Immune reconstitution inflammatory syndrome Diseases 0.000 description 2
- 102000012011 Isocitrate Dehydrogenase Human genes 0.000 description 2
- 108010075869 Isocitrate Dehydrogenase Proteins 0.000 description 2
- AGPKZVBTJJNPAG-WHFBIAKZSA-N L-isoleucine Chemical compound CC[C@H](C)[C@H](N)C(O)=O AGPKZVBTJJNPAG-WHFBIAKZSA-N 0.000 description 2
- BACYUWVYYTXETD-UHFFFAOYSA-N N-Lauroylsarcosine Chemical compound CCCCCCCCCCCC(=O)N(C)CC(O)=O BACYUWVYYTXETD-UHFFFAOYSA-N 0.000 description 2
- 108091005804 Peptidases Proteins 0.000 description 2
- 102000035195 Peptidases Human genes 0.000 description 2
- 241000288935 Platyrrhini Species 0.000 description 2
- 239000002202 Polyethylene glycol Substances 0.000 description 2
- 108020004511 Recombinant DNA Proteins 0.000 description 2
- 229920005654 Sephadex Polymers 0.000 description 2
- 239000012507 Sephadex™ Substances 0.000 description 2
- MTCFGRXMJLQNBG-UHFFFAOYSA-N Serine Natural products OCC(N)C(O)=O MTCFGRXMJLQNBG-UHFFFAOYSA-N 0.000 description 2
- 108091081024 Start codon Proteins 0.000 description 2
- 108010008038 Synthetic Vaccines Proteins 0.000 description 2
- KZSNJWFQEVHDMF-UHFFFAOYSA-N Valine Chemical compound CC(C)C(N)C(O)=O KZSNJWFQEVHDMF-UHFFFAOYSA-N 0.000 description 2
- 230000009471 action Effects 0.000 description 2
- 239000004480 active ingredient Substances 0.000 description 2
- 239000013543 active substance Substances 0.000 description 2
- 239000002671 adjuvant Substances 0.000 description 2
- 125000000539 amino acid group Chemical group 0.000 description 2
- 229940043376 ammonium acetate Drugs 0.000 description 2
- 235000019257 ammonium acetate Nutrition 0.000 description 2
- ODKSFYDXXFIFQN-UHFFFAOYSA-N arginine Natural products OC(=O)C(N)CCCNC(N)=N ODKSFYDXXFIFQN-UHFFFAOYSA-N 0.000 description 2
- 125000000637 arginyl group Chemical class N[C@@H](CCCNC(N)=N)C(=O)* 0.000 description 2
- 238000011948 assay development Methods 0.000 description 2
- 210000003719 b-lymphocyte Anatomy 0.000 description 2
- 108010058966 bacteriophage T7 induced DNA polymerase Proteins 0.000 description 2
- 210000000941 bile Anatomy 0.000 description 2
- 239000011230 binding agent Substances 0.000 description 2
- 230000004071 biological effect Effects 0.000 description 2
- UDSAIICHUKSCKT-UHFFFAOYSA-N bromophenol blue Chemical compound C1=C(Br)C(O)=C(Br)C=C1C1(C=2C=C(Br)C(O)=C(Br)C=2)C2=CC=CC=C2S(=O)(=O)O1 UDSAIICHUKSCKT-UHFFFAOYSA-N 0.000 description 2
- 244000309466 calf Species 0.000 description 2
- 210000000234 capsid Anatomy 0.000 description 2
- 239000001768 carboxy methyl cellulose Substances 0.000 description 2
- 235000010948 carboxy methyl cellulose Nutrition 0.000 description 2
- 239000008112 carboxymethyl-cellulose Substances 0.000 description 2
- 230000015556 catabolic process Effects 0.000 description 2
- -1 cationic lipid Chemical class 0.000 description 2
- 230000001186 cumulative effect Effects 0.000 description 2
- 238000006731 degradation reaction Methods 0.000 description 2
- 238000011161 development Methods 0.000 description 2
- LOKCTEFSRHRXRJ-UHFFFAOYSA-I dipotassium trisodium dihydrogen phosphate hydrogen phosphate dichloride Chemical compound P(=O)(O)(O)[O-].[K+].P(=O)(O)([O-])[O-].[Na+].[Na+].[Cl-].[K+].[Cl-].[Na+] LOKCTEFSRHRXRJ-UHFFFAOYSA-I 0.000 description 2
- 238000001493 electron microscopy Methods 0.000 description 2
- ZMMJGEGLRURXTF-UHFFFAOYSA-N ethidium bromide Chemical compound [Br-].C12=CC(N)=CC=C2C2=CC=C(N)C=C2[N+](CC)=C1C1=CC=CC=C1 ZMMJGEGLRURXTF-UHFFFAOYSA-N 0.000 description 2
- 229960005542 ethidium bromide Drugs 0.000 description 2
- 239000000284 extract Substances 0.000 description 2
- 108010074605 gamma-Globulins Proteins 0.000 description 2
- 102000006640 gamma-Glutamyltransferase Human genes 0.000 description 2
- 238000001502 gel electrophoresis Methods 0.000 description 2
- 239000011544 gradient gel Substances 0.000 description 2
- 244000144993 groups of animals Species 0.000 description 2
- ZJYYHGLJYGJLLN-UHFFFAOYSA-N guanidinium thiocyanate Chemical compound SC#N.NC(N)=N ZJYYHGLJYGJLLN-UHFFFAOYSA-N 0.000 description 2
- 238000003306 harvesting Methods 0.000 description 2
- 208000005252 hepatitis A Diseases 0.000 description 2
- 230000036732 histological change Effects 0.000 description 2
- 238000001802 infusion Methods 0.000 description 2
- 239000004615 ingredient Substances 0.000 description 2
- 238000010255 intramuscular injection Methods 0.000 description 2
- 239000007927 intramuscular injection Substances 0.000 description 2
- 238000007912 intraperitoneal administration Methods 0.000 description 2
- 150000002500 ions Chemical class 0.000 description 2
- 238000002955 isolation Methods 0.000 description 2
- RCRODHONKLSMIF-UHFFFAOYSA-N isosuberenol Natural products O1C(=O)C=CC2=C1C=C(OC)C(CC(O)C(C)=C)=C2 RCRODHONKLSMIF-UHFFFAOYSA-N 0.000 description 2
- 108010045069 keyhole-limpet hemocyanin Proteins 0.000 description 2
- 229940059904 light mineral oil Drugs 0.000 description 2
- 238000004811 liquid chromatography Methods 0.000 description 2
- 238000012317 liver biopsy Methods 0.000 description 2
- 125000003588 lysine group Chemical group [H]N([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])(N([H])[H])C(*)=O 0.000 description 2
- 229920002521 macromolecule Polymers 0.000 description 2
- HQKMJHAJHXVSDF-UHFFFAOYSA-L magnesium stearate Chemical compound [Mg+2].CCCCCCCCCCCCCCCCCC([O-])=O.CCCCCCCCCCCCCCCCCC([O-])=O HQKMJHAJHXVSDF-UHFFFAOYSA-L 0.000 description 2
- 239000002609 medium Substances 0.000 description 2
- 229920000609 methyl cellulose Polymers 0.000 description 2
- 239000001923 methylcellulose Substances 0.000 description 2
- 235000010981 methylcellulose Nutrition 0.000 description 2
- 230000000877 morphologic effect Effects 0.000 description 2
- 238000013188 needle biopsy Methods 0.000 description 2
- 230000008520 organization Effects 0.000 description 2
- 230000036961 partial effect Effects 0.000 description 2
- 239000008188 pellet Substances 0.000 description 2
- 230000000737 periodic effect Effects 0.000 description 2
- YBYRMVIVWMBXKQ-UHFFFAOYSA-N phenylmethanesulfonyl fluoride Chemical compound FS(=O)(=O)CC1=CC=CC=C1 YBYRMVIVWMBXKQ-UHFFFAOYSA-N 0.000 description 2
- 229920001308 poly(aminoacid) Polymers 0.000 description 2
- 229920001200 poly(ethylene-vinyl acetate) Polymers 0.000 description 2
- 238000002264 polyacrylamide gel electrophoresis Methods 0.000 description 2
- 229920000728 polyester Polymers 0.000 description 2
- 229920001223 polyethylene glycol Polymers 0.000 description 2
- 238000012808 pre-inoculation Methods 0.000 description 2
- 238000011321 prophylaxis Methods 0.000 description 2
- 230000006337 proteolytic cleavage Effects 0.000 description 2
- 229940124551 recombinant vaccine Drugs 0.000 description 2
- 239000011347 resin Substances 0.000 description 2
- 229920005989 resin Polymers 0.000 description 2
- 108700004121 sarkosyl Proteins 0.000 description 2
- 238000012216 screening Methods 0.000 description 2
- 238000013207 serial dilution Methods 0.000 description 2
- 210000004989 spleen cell Anatomy 0.000 description 2
- 238000007920 subcutaneous administration Methods 0.000 description 2
- 208000024891 symptom Diseases 0.000 description 2
- 238000013519 translation Methods 0.000 description 2
- 238000011144 upstream manufacturing Methods 0.000 description 2
- 238000005406 washing Methods 0.000 description 2
- LNAZSHAWQACDHT-XIYTZBAFSA-N (2r,3r,4s,5r,6s)-4,5-dimethoxy-2-(methoxymethyl)-3-[(2s,3r,4s,5r,6r)-3,4,5-trimethoxy-6-(methoxymethyl)oxan-2-yl]oxy-6-[(2r,3r,4s,5r,6r)-4,5,6-trimethoxy-2-(methoxymethyl)oxan-3-yl]oxyoxane Chemical compound CO[C@@H]1[C@@H](OC)[C@H](OC)[C@@H](COC)O[C@H]1O[C@H]1[C@H](OC)[C@@H](OC)[C@H](O[C@H]2[C@@H]([C@@H](OC)[C@H](OC)O[C@@H]2COC)OC)O[C@@H]1COC LNAZSHAWQACDHT-XIYTZBAFSA-N 0.000 description 1
- IXPNQXFRVYWDDI-UHFFFAOYSA-N 1-methyl-2,4-dioxo-1,3-diazinane-5-carboximidamide Chemical compound CN1CC(C(N)=N)C(=O)NC1=O IXPNQXFRVYWDDI-UHFFFAOYSA-N 0.000 description 1
- NKDFYOWSKOHCCO-YPVLXUMRSA-N 20-hydroxyecdysone Chemical compound C1[C@@H](O)[C@@H](O)C[C@]2(C)[C@@H](CC[C@@]3([C@@H]([C@@](C)(O)[C@H](O)CCC(C)(O)C)CC[C@]33O)C)C3=CC(=O)[C@@H]21 NKDFYOWSKOHCCO-YPVLXUMRSA-N 0.000 description 1
- FMVWVPAXPVSWER-UHFFFAOYSA-N 5-(2-methylpropyl)-3-phenyl-2-sulfanylideneimidazolidin-4-one Chemical compound O=C1C(CC(C)C)NC(=S)N1C1=CC=CC=C1 FMVWVPAXPVSWER-UHFFFAOYSA-N 0.000 description 1
- XGPFPXALZVOKRI-UHFFFAOYSA-N 5-methyl-3-phenyl-2-sulfanylideneimidazolidin-4-one Chemical compound O=C1C(C)NC(=S)N1C1=CC=CC=C1 XGPFPXALZVOKRI-UHFFFAOYSA-N 0.000 description 1
- 244000215068 Acacia senegal Species 0.000 description 1
- 229920000936 Agarose Polymers 0.000 description 1
- 108010088751 Albumins Proteins 0.000 description 1
- 102000009027 Albumins Human genes 0.000 description 1
- 206010002091 Anaesthesia Diseases 0.000 description 1
- 241000282709 Aotus trivirgatus Species 0.000 description 1
- 108010039627 Aprotinin Proteins 0.000 description 1
- DJIMLSXHXKWADV-CIUDSAMLSA-N Asn-Leu-Ser Chemical compound OC[C@@H](C(O)=O)NC(=O)[C@H](CC(C)C)NC(=O)[C@@H](N)CC(N)=O DJIMLSXHXKWADV-CIUDSAMLSA-N 0.000 description 1
- 241000713838 Avian myeloblastosis virus Species 0.000 description 1
- 101100228196 Caenorhabditis elegans gly-4 gene Proteins 0.000 description 1
- 108090000565 Capsid Proteins Proteins 0.000 description 1
- OKTJSMMVPCPJKN-UHFFFAOYSA-N Carbon Chemical compound [C] OKTJSMMVPCPJKN-UHFFFAOYSA-N 0.000 description 1
- 102100023321 Ceruloplasmin Human genes 0.000 description 1
- 241000282552 Chlorocebus aethiops Species 0.000 description 1
- 108091026890 Coding region Proteins 0.000 description 1
- 239000003155 DNA primer Substances 0.000 description 1
- 230000006820 DNA synthesis Effects 0.000 description 1
- 238000001061 Dunnett's test Methods 0.000 description 1
- 101150013191 E gene Proteins 0.000 description 1
- 238000012286 ELISA Assay Methods 0.000 description 1
- 241000724791 Filamentous phage Species 0.000 description 1
- 241001295925 Gegenes Species 0.000 description 1
- 229920000084 Gum arabic Polymers 0.000 description 1
- 241000711549 Hepacivirus C Species 0.000 description 1
- 241000700721 Hepatitis B virus Species 0.000 description 1
- 208000005176 Hepatitis C Diseases 0.000 description 1
- 208000005331 Hepatitis D Diseases 0.000 description 1
- 241001622557 Hesperia Species 0.000 description 1
- 101000581940 Homo sapiens Napsin-A Proteins 0.000 description 1
- 108010001336 Horseradish Peroxidase Proteins 0.000 description 1
- 238000012695 Interfacial polymerization Methods 0.000 description 1
- WHUUTDBJXJRKMK-VKHMYHEASA-N L-glutamic acid Chemical compound OC(=O)[C@@H](N)CCC(O)=O WHUUTDBJXJRKMK-VKHMYHEASA-N 0.000 description 1
- HNDVDQJCIGZPNO-YFKPBYRVSA-N L-histidine Chemical compound OC(=O)[C@@H](N)CC1=CN=CN1 HNDVDQJCIGZPNO-YFKPBYRVSA-N 0.000 description 1
- KZSNJWFQEVHDMF-BYPYZUCNSA-N L-valine Chemical compound CC(C)[C@H](N)C(O)=O KZSNJWFQEVHDMF-BYPYZUCNSA-N 0.000 description 1
- GUBGYTABKSRVRQ-QKKXKWKRSA-N Lactose Natural products OC[C@H]1O[C@@H](O[C@H]2[C@H](O)[C@@H](O)C(O)O[C@@H]2CO)[C@H](O)[C@@H](O)[C@H]1O GUBGYTABKSRVRQ-QKKXKWKRSA-N 0.000 description 1
- 239000004907 Macro-emulsion Substances 0.000 description 1
- 201000005505 Measles Diseases 0.000 description 1
- 101710134502 Mgp-operon protein 3 Proteins 0.000 description 1
- BKAYIFDRRZZKNF-VIFPVBQESA-N N-acetylcarnosine Chemical compound CC(=O)NCCC(=O)N[C@H](C(O)=O)CC1=CN=CN1 BKAYIFDRRZZKNF-VIFPVBQESA-N 0.000 description 1
- 102100027343 Napsin-A Human genes 0.000 description 1
- 206010028980 Neoplasm Diseases 0.000 description 1
- 101100205180 Neurospora crassa (strain ATCC 24698 / 74-OR23-1A / CBS 708.71 / DSM 1257 / FGSC 987) leu-6 gene Proteins 0.000 description 1
- 101150009852 ORF2 gene Proteins 0.000 description 1
- 239000002033 PVDF binder Substances 0.000 description 1
- 102000004160 Phosphoric Monoester Hydrolases Human genes 0.000 description 1
- 108090000608 Phosphoric Monoester Hydrolases Proteins 0.000 description 1
- 229920002594 Polyethylene Glycol 8000 Polymers 0.000 description 1
- 108010039918 Polylysine Proteins 0.000 description 1
- 229920001213 Polysorbate 20 Polymers 0.000 description 1
- 239000004793 Polystyrene Substances 0.000 description 1
- 102000007327 Protamines Human genes 0.000 description 1
- 108010007568 Protamines Proteins 0.000 description 1
- 239000004365 Protease Substances 0.000 description 1
- 108010076504 Protein Sorting Signals Proteins 0.000 description 1
- 239000012614 Q-Sepharose Substances 0.000 description 1
- 206010037742 Rabies Diseases 0.000 description 1
- 241000220317 Rosa Species 0.000 description 1
- 241000288956 Saguinus mystax Species 0.000 description 1
- 241000282696 Saimiri sciureus Species 0.000 description 1
- 241000256251 Spodoptera frugiperda Species 0.000 description 1
- 229920002472 Starch Polymers 0.000 description 1
- 238000000692 Student's t-test Methods 0.000 description 1
- 229930006000 Sucrose Natural products 0.000 description 1
- CZMRCDWAGMRECN-UGDNZRGBSA-N Sucrose Chemical compound O[C@H]1[C@H](O)[C@@H](CO)O[C@@]1(CO)O[C@@H]1[C@H](O)[C@@H](O)[C@H](O)[C@@H](CO)O1 CZMRCDWAGMRECN-UGDNZRGBSA-N 0.000 description 1
- 239000012505 Superdex™ Substances 0.000 description 1
- 108020005038 Terminator Codon Proteins 0.000 description 1
- 108090000340 Transaminases Proteins 0.000 description 1
- 108090000631 Trypsin Proteins 0.000 description 1
- 102000004142 Trypsin Human genes 0.000 description 1
- 241000700618 Vaccinia virus Species 0.000 description 1
- 206010046865 Vaccinia virus infection Diseases 0.000 description 1
- 108700005077 Viral Genes Proteins 0.000 description 1
- 238000001793 Wilcoxon signed-rank test Methods 0.000 description 1
- 230000002159 abnormal effect Effects 0.000 description 1
- 235000010489 acacia gum Nutrition 0.000 description 1
- 239000000205 acacia gum Substances 0.000 description 1
- 238000007792 addition Methods 0.000 description 1
- 239000003463 adsorbent Substances 0.000 description 1
- 230000002411 adverse Effects 0.000 description 1
- 238000001042 affinity chromatography Methods 0.000 description 1
- BFNBIHQBYMNNAN-UHFFFAOYSA-N ammonium sulfate Chemical class N.N.OS(O)(=O)=O BFNBIHQBYMNNAN-UHFFFAOYSA-N 0.000 description 1
- 230000037005 anaesthesia Effects 0.000 description 1
- 230000003444 anaesthetic effect Effects 0.000 description 1
- 238000010171 animal model Methods 0.000 description 1
- 230000000840 anti-viral effect Effects 0.000 description 1
- 238000013459 approach Methods 0.000 description 1
- 229960004405 aprotinin Drugs 0.000 description 1
- 229910052786 argon Inorganic materials 0.000 description 1
- 238000001574 biopsy Methods 0.000 description 1
- 239000001045 blue dye Substances 0.000 description 1
- 230000037396 body weight Effects 0.000 description 1
- 230000003139 buffering effect Effects 0.000 description 1
- DQXBYHZEEUGOBF-UHFFFAOYSA-N but-3-enoic acid;ethene Chemical compound C=C.OC(=O)CC=C DQXBYHZEEUGOBF-UHFFFAOYSA-N 0.000 description 1
- 201000011510 cancer Diseases 0.000 description 1
- 150000001720 carbohydrates Chemical class 0.000 description 1
- 229910052799 carbon Inorganic materials 0.000 description 1
- 239000013553 cell monolayer Substances 0.000 description 1
- 210000003855 cell nucleus Anatomy 0.000 description 1
- 210000001175 cerebrospinal fluid Anatomy 0.000 description 1
- 230000008859 change Effects 0.000 description 1
- 239000003795 chemical substances by application Substances 0.000 description 1
- YTRQFSDWAXHJCC-UHFFFAOYSA-N chloroform;phenol Chemical compound ClC(Cl)Cl.OC1=CC=CC=C1 YTRQFSDWAXHJCC-UHFFFAOYSA-N 0.000 description 1
- 239000003593 chromogenic compound Substances 0.000 description 1
- 210000001728 clone cell Anatomy 0.000 description 1
- 239000013599 cloning vector Substances 0.000 description 1
- 238000004040 coloring Methods 0.000 description 1
- 238000004440 column chromatography Methods 0.000 description 1
- 230000000052 comparative effect Effects 0.000 description 1
- 230000002860 competitive effect Effects 0.000 description 1
- 238000002967 competitive immunoassay Methods 0.000 description 1
- 238000013270 controlled release Methods 0.000 description 1
- 230000009260 cross reactivity Effects 0.000 description 1
- 239000012228 culture supernatant Substances 0.000 description 1
- 230000009089 cytolysis Effects 0.000 description 1
- 230000001086 cytosolic effect Effects 0.000 description 1
- 230000003111 delayed effect Effects 0.000 description 1
- 238000004925 denaturation Methods 0.000 description 1
- 230000036425 denaturation Effects 0.000 description 1
- 230000001419 dependent effect Effects 0.000 description 1
- 230000008021 deposition Effects 0.000 description 1
- 238000001212 derivatisation Methods 0.000 description 1
- 238000010586 diagram Methods 0.000 description 1
- 239000012153 distilled water Substances 0.000 description 1
- 239000002552 dosage form Substances 0.000 description 1
- 231100000673 dose–response relationship Toxicity 0.000 description 1
- 229940079593 drug Drugs 0.000 description 1
- 238000012377 drug delivery Methods 0.000 description 1
- 241001493065 dsRNA viruses Species 0.000 description 1
- 238000000635 electron micrograph Methods 0.000 description 1
- 210000004407 endothelial cell of postcapillary venule of lymph node Anatomy 0.000 description 1
- 239000005038 ethylene vinyl acetate Substances 0.000 description 1
- 238000011156 evaluation Methods 0.000 description 1
- 239000012091 fetal bovine serum Substances 0.000 description 1
- 238000007667 floating Methods 0.000 description 1
- 238000005194 fractionation Methods 0.000 description 1
- 238000001415 gene therapy Methods 0.000 description 1
- 230000002068 genetic effect Effects 0.000 description 1
- 238000010353 genetic engineering Methods 0.000 description 1
- 235000013922 glutamic acid Nutrition 0.000 description 1
- 239000004220 glutamic acid Substances 0.000 description 1
- PCHJSUWPFVWCPO-UHFFFAOYSA-N gold Chemical compound [Au] PCHJSUWPFVWCPO-UHFFFAOYSA-N 0.000 description 1
- 238000004128 high performance liquid chromatography Methods 0.000 description 1
- HNDVDQJCIGZPNO-UHFFFAOYSA-N histidine Natural products OC(=O)C(N)CC1=CN=CN1 HNDVDQJCIGZPNO-UHFFFAOYSA-N 0.000 description 1
- 238000002744 homologous recombination Methods 0.000 description 1
- 230000006801 homologous recombination Effects 0.000 description 1
- 239000000017 hydrogel Substances 0.000 description 1
- 229920003063 hydroxymethyl cellulose Polymers 0.000 description 1
- 229940031574 hydroxymethyl cellulose Drugs 0.000 description 1
- 230000001900 immune effect Effects 0.000 description 1
- 230000028993 immune response Effects 0.000 description 1
- 230000000899 immune system response Effects 0.000 description 1
- 230000036039 immunity Effects 0.000 description 1
- 238000010166 immunofluorescence Methods 0.000 description 1
- 230000016784 immunoglobulin production Effects 0.000 description 1
- 229940072221 immunoglobulins Drugs 0.000 description 1
- 230000002055 immunohistochemical effect Effects 0.000 description 1
- 238000000338 in vitro Methods 0.000 description 1
- 238000011065 in-situ storage Methods 0.000 description 1
- 238000010348 incorporation Methods 0.000 description 1
- 230000006698 induction Effects 0.000 description 1
- 230000001939 inductive effect Effects 0.000 description 1
- 239000012678 infectious agent Substances 0.000 description 1
- 230000002757 inflammatory effect Effects 0.000 description 1
- ZPNFWUPYTFPOJU-LPYSRVMUSA-N iniprol Chemical compound C([C@H]1C(=O)NCC(=O)NCC(=O)N[C@H]2CSSC[C@H]3C(=O)N[C@@H](CCCCN)C(=O)N[C@@H](C)C(=O)N[C@@H](CCCNC(N)=N)C(=O)N[C@H](C(N[C@H](C(=O)N[C@@H](CCCNC(N)=N)C(=O)N[C@@H](CC=4C=CC(O)=CC=4)C(=O)N[C@@H](CC=4C=CC=CC=4)C(=O)N[C@@H](CC=4C=CC(O)=CC=4)C(=O)N[C@@H](CC(N)=O)C(=O)N[C@@H](C)C(=O)N[C@@H](CCCCN)C(=O)N[C@@H](C)C(=O)NCC(=O)N[C@@H](CC(C)C)C(=O)N[C@@H](CSSC[C@H](NC(=O)[C@H](CC(O)=O)NC(=O)[C@H](CCC(O)=O)NC(=O)[C@H](C)NC(=O)[C@H](CO)NC(=O)[C@H](CCCCN)NC(=O)[C@H](CC=4C=CC=CC=4)NC(=O)[C@H](CC(N)=O)NC(=O)[C@H](CC(N)=O)NC(=O)[C@H](CCCNC(N)=N)NC(=O)[C@H](CCCCN)NC(=O)[C@H](C)NC(=O)[C@H](CCCNC(N)=N)NC2=O)C(=O)N[C@@H](CCSC)C(=O)N[C@@H](CCCNC(N)=N)C(=O)N[C@@H]([C@@H](C)O)C(=O)N[C@@H](CSSC[C@H](NC(=O)[C@H](CC=2C=CC=CC=2)NC(=O)[C@H](CC(O)=O)NC(=O)[C@H]2N(CCC2)C(=O)[C@@H](N)CCCNC(N)=N)C(=O)N[C@@H](CC(C)C)C(=O)N[C@@H](CCC(O)=O)C(=O)N2[C@@H](CCC2)C(=O)N2[C@@H](CCC2)C(=O)N[C@@H](CC=2C=CC(O)=CC=2)C(=O)N[C@@H]([C@@H](C)O)C(=O)NCC(=O)N2[C@@H](CCC2)C(=O)N3)C(=O)NCC(=O)NCC(=O)N[C@@H](C)C(O)=O)C(=O)N[C@@H](CCC(N)=O)C(=O)N[C@H](C(=O)N[C@@H](CC=2C=CC=CC=2)C(=O)N[C@H](C(=O)N1)C(C)C)[C@@H](C)O)[C@@H](C)CC)=O)[C@@H](C)CC)C1=CC=C(O)C=C1 ZPNFWUPYTFPOJU-LPYSRVMUSA-N 0.000 description 1
- 238000003780 insertion Methods 0.000 description 1
- 230000037431 insertion Effects 0.000 description 1
- 238000009434 installation Methods 0.000 description 1
- 238000005342 ion exchange Methods 0.000 description 1
- 238000004255 ion exchange chromatography Methods 0.000 description 1
- 238000001155 isoelectric focusing Methods 0.000 description 1
- AGPKZVBTJJNPAG-UHFFFAOYSA-N isoleucine Natural products CCC(C)C(N)C(O)=O AGPKZVBTJJNPAG-UHFFFAOYSA-N 0.000 description 1
- 229960000310 isoleucine Drugs 0.000 description 1
- 239000008101 lactose Substances 0.000 description 1
- 239000002502 liposome Substances 0.000 description 1
- 239000007788 liquid Substances 0.000 description 1
- 239000007791 liquid phase Substances 0.000 description 1
- 238000000464 low-speed centrifugation Methods 0.000 description 1
- 239000012139 lysis buffer Substances 0.000 description 1
- 235000019359 magnesium stearate Nutrition 0.000 description 1
- 238000001819 mass spectrum Methods 0.000 description 1
- 239000011159 matrix material Substances 0.000 description 1
- 235000019988 mead Nutrition 0.000 description 1
- 238000005259 measurement Methods 0.000 description 1
- 239000004530 micro-emulsion Substances 0.000 description 1
- 244000005700 microbiome Species 0.000 description 1
- 239000004005 microsphere Substances 0.000 description 1
- 238000007392 microtiter assay Methods 0.000 description 1
- 150000007522 mineralic acids Chemical class 0.000 description 1
- 239000002808 molecular sieve Substances 0.000 description 1
- 238000012544 monitoring process Methods 0.000 description 1
- 238000004264 monolayer culture Methods 0.000 description 1
- 238000002703 mutagenesis Methods 0.000 description 1
- 231100000350 mutagenesis Toxicity 0.000 description 1
- 239000002088 nanocapsule Substances 0.000 description 1
- 239000002105 nanoparticle Substances 0.000 description 1
- 239000006199 nebulizer Substances 0.000 description 1
- 230000017074 necrotic cell death Effects 0.000 description 1
- 229910052757 nitrogen Inorganic materials 0.000 description 1
- 230000000422 nocturnal effect Effects 0.000 description 1
- 230000036963 noncompetitive effect Effects 0.000 description 1
- 150000007524 organic acids Chemical class 0.000 description 1
- 235000005985 organic acids Nutrition 0.000 description 1
- 230000003204 osmotic effect Effects 0.000 description 1
- 230000002018 overexpression Effects 0.000 description 1
- 238000004091 panning Methods 0.000 description 1
- 210000005259 peripheral blood Anatomy 0.000 description 1
- 239000011886 peripheral blood Substances 0.000 description 1
- 235000020030 perry Nutrition 0.000 description 1
- 239000000825 pharmaceutical preparation Substances 0.000 description 1
- 230000004962 physiological condition Effects 0.000 description 1
- 210000004910 pleural fluid Anatomy 0.000 description 1
- 229920000747 poly(lactic acid) Polymers 0.000 description 1
- 229920003229 poly(methyl methacrylate) Polymers 0.000 description 1
- 229920000656 polylysine Polymers 0.000 description 1
- 229920000642 polymer Polymers 0.000 description 1
- 238000003752 polymerase chain reaction Methods 0.000 description 1
- 239000004926 polymethyl methacrylate Substances 0.000 description 1
- 239000000256 polyoxyethylene sorbitan monolaurate Substances 0.000 description 1
- 235000010486 polyoxyethylene sorbitan monolaurate Nutrition 0.000 description 1
- 229920002223 polystyrene Polymers 0.000 description 1
- 229920002981 polyvinylidene fluoride Polymers 0.000 description 1
- 238000012809 post-inoculation Methods 0.000 description 1
- 230000003389 potentiating effect Effects 0.000 description 1
- 238000004321 preservation Methods 0.000 description 1
- 238000004393 prognosis Methods 0.000 description 1
- 210000001236 prokaryotic cell Anatomy 0.000 description 1
- 229950008679 protamine sulfate Drugs 0.000 description 1
- 235000019833 protease Nutrition 0.000 description 1
- 235000019419 proteases Nutrition 0.000 description 1
- 239000012460 protein solution Substances 0.000 description 1
- 230000002797 proteolythic effect Effects 0.000 description 1
- HNJBEVLQSNELDL-UHFFFAOYSA-N pyrrolidin-2-one Chemical compound O=C1CCCN1 HNJBEVLQSNELDL-UHFFFAOYSA-N 0.000 description 1
- 238000011002 quantification Methods 0.000 description 1
- 238000003127 radioimmunoassay Methods 0.000 description 1
- 239000002994 raw material Substances 0.000 description 1
- 238000011084 recovery Methods 0.000 description 1
- 230000010076 replication Effects 0.000 description 1
- 238000011160 research Methods 0.000 description 1
- 230000001177 retroviral effect Effects 0.000 description 1
- 238000004007 reversed phase HPLC Methods 0.000 description 1
- 239000012723 sample buffer Substances 0.000 description 1
- 238000005070 sampling Methods 0.000 description 1
- 230000003248 secreting effect Effects 0.000 description 1
- 238000005204 segregation Methods 0.000 description 1
- 238000000926 separation method Methods 0.000 description 1
- 238000007493 shaping process Methods 0.000 description 1
- 239000007974 sodium acetate buffer Substances 0.000 description 1
- 235000010413 sodium alginate Nutrition 0.000 description 1
- 239000000661 sodium alginate Substances 0.000 description 1
- 229940005550 sodium alginate Drugs 0.000 description 1
- URGAHOPLAPQHLN-UHFFFAOYSA-N sodium aluminosilicate Chemical compound [Na+].[Al+3].[O-][Si]([O-])=O.[O-][Si]([O-])=O URGAHOPLAPQHLN-UHFFFAOYSA-N 0.000 description 1
- 238000002415 sodium dodecyl sulfate polyacrylamide gel electrophoresis Methods 0.000 description 1
- 239000002904 solvent Substances 0.000 description 1
- 238000001179 sorption measurement Methods 0.000 description 1
- 230000009870 specific binding Effects 0.000 description 1
- 238000001228 spectrum Methods 0.000 description 1
- 239000012192 staining solution Substances 0.000 description 1
- 239000012086 standard solution Substances 0.000 description 1
- 239000008107 starch Substances 0.000 description 1
- 235000019698 starch Nutrition 0.000 description 1
- 230000001954 sterilising effect Effects 0.000 description 1
- 239000000126 substance Substances 0.000 description 1
- 239000005720 sucrose Substances 0.000 description 1
- 230000004083 survival effect Effects 0.000 description 1
- 239000000454 talc Substances 0.000 description 1
- 229910052623 talc Inorganic materials 0.000 description 1
- 235000012222 talc Nutrition 0.000 description 1
- 229960000814 tetanus toxoid Drugs 0.000 description 1
- 229940124597 therapeutic agent Drugs 0.000 description 1
- 210000001519 tissue Anatomy 0.000 description 1
- 102000014898 transaminase activity proteins Human genes 0.000 description 1
- 238000001890 transfection Methods 0.000 description 1
- 230000014621 translational initiation Effects 0.000 description 1
- 239000012588 trypsin Substances 0.000 description 1
- 241000701161 unidentified adenovirus Species 0.000 description 1
- 241001529453 unidentified herpesvirus Species 0.000 description 1
- 210000002700 urine Anatomy 0.000 description 1
- 208000007089 vaccinia Diseases 0.000 description 1
- 238000010200 validation analysis Methods 0.000 description 1
- 239000004474 valine Substances 0.000 description 1
- 239000012808 vapor phase Substances 0.000 description 1
- 229920002554 vinyl polymer Polymers 0.000 description 1
- 230000007502 viral entry Effects 0.000 description 1
- 230000029812 viral genome replication Effects 0.000 description 1
- 239000013603 viral vector Substances 0.000 description 1
- 230000003313 weakening effect Effects 0.000 description 1
- DGVVWUTYPXICAM-UHFFFAOYSA-N β‐Mercaptoethanol Chemical compound OCCS DGVVWUTYPXICAM-UHFFFAOYSA-N 0.000 description 1
Classifications
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K14/00—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof
- C07K14/005—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof from viruses
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61P—SPECIFIC THERAPEUTIC ACTIVITY OF CHEMICAL COMPOUNDS OR MEDICINAL PREPARATIONS
- A61P1/00—Drugs for disorders of the alimentary tract or the digestive system
- A61P1/16—Drugs for disorders of the alimentary tract or the digestive system for liver or gallbladder disorders, e.g. hepatoprotective agents, cholagogues, litholytics
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61P—SPECIFIC THERAPEUTIC ACTIVITY OF CHEMICAL COMPOUNDS OR MEDICINAL PREPARATIONS
- A61P31/00—Antiinfectives, i.e. antibiotics, antiseptics, chemotherapeutics
- A61P31/12—Antivirals
- A61P31/14—Antivirals for RNA viruses
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61P—SPECIFIC THERAPEUTIC ACTIVITY OF CHEMICAL COMPOUNDS OR MEDICINAL PREPARATIONS
- A61P31/00—Antiinfectives, i.e. antibiotics, antiseptics, chemotherapeutics
- A61P31/12—Antivirals
- A61P31/20—Antivirals for DNA viruses
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K39/00—Medicinal preparations containing antigens or antibodies
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2770/00—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA ssRNA viruses positive-sense
- C12N2770/00011—Details
- C12N2770/28011—Hepeviridae
- C12N2770/28111—Hepevirus, e.g. hepatitis E virus
- C12N2770/28122—New viral proteins or individual genes, new structural or functional aspects of known viral proteins or genes
-
- G—PHYSICS
- G01—MEASURING; TESTING
- G01N—INVESTIGATING OR ANALYSING MATERIALS BY DETERMINING THEIR CHEMICAL OR PHYSICAL PROPERTIES
- G01N2333/00—Assays involving biological materials from specific organisms or of a specific nature
- G01N2333/005—Assays involving biological materials from specific organisms or of a specific nature from viruses
- G01N2333/08—RNA viruses
Description
- Gebiet der Erfindung
- Die Erfindung liegt im Gebiet der Hepatitis-Virologie. Insbesondere betrifft die Erfindung rekombinante Proteine, die von einem enteral übertragenen Pakistani-Stamm von Hepatitis E, SAR-55, abgeleitet sind, und Verfahren zum Nachweis von Antikörpern gegen Hepatitis-E-Virus und Vakzin-Anwendungen, die diese Proteine verwenden.
- Hintergrund der Erfindung
- Epidemien von Hepatitis E, einer enteral übertragenen Nicht-A/Nicht-B-Hepatitis, sind in Asien, Afrika und Zentralamerika berichtet worden (Balayan, M. S. (1987), Soviet Medical Reviews, Sektion E, Virology Reviews, Zhdanov, O-V. M. (Hrsg.), Chur, Schweiz: Harwood Academic Publishers, Band 2, 235–261; Purcell, R. G. et al. (1988) in Zuckerman, A. J. (Hrsg.), "Viral Hepatitis and Liver Disease", New York: Alan R. Liss, 131–137; Bradley, D. W. (1990), British Medical Bulletin, 46: 442–461; Ticehurst, J. R. (1991) in Hollinger, F. B., Lemon, S. M., Margolis, H. S. (Hrsg.): "Viral Hepatitis and Liver Disease", Williams and Wilkins, Baltimore, 501–513). Fälle von sporadischer Hepatitis, mutmaßlich Hepatitis E, machen bis zu 90% der berichteten Hepatitis in Ländern aus, in denen Hepatitis E-Virus (HEV) endemisch ist. Das Bedürfnis für eine Entwicklung eines serologischen Tests für den Nachweis von Anti-HEV-Antikörpern in den Seren von infizierten Individuen ist im Fachgebiet weithin anerkannt, aber die sehr geringe Konzentration an HEV, die von infizierten Menschen oder Tieren ausgeschieden wird, machte es unmöglich, solches HEV als Quelle an Antigen für serologische Tests zu verwenden, und obwohl eingeschränkter Erfolg bei der Propagierung von HEV in Zellkultur berichtet wurde (Huang, R. T. et al. (1992), J. Gen. Virol., 73: 1143–1148), ist Zellkultur momentan zu ineffizient, um die Mengen an Antigen zu produzieren, die für serologische Tests benötigt werden.
- Kürzlich haben größere Anstrengungen weltweit, virale genomische Sequenzen zu identifizieren, die mit Hepatitis E assoziiert sind, zu der Klonierung der Genome einer begrenzten Anzahl an Stämmen von HEV geführt (Tam, A. W. et al. (1991), Virology, 185: 120–131; Tsarev, S. A. et al. (1992), Proc. Natl. Acad. Sci. USA, 89: 559–563; Fry, K. E. et al. (1992), Virus Genes, 6: 173–185). Eine Analyse der DNA-Sequenzen führte Forscher dazu, anzunehmen, dass das HEV-Genom in drei offenen Leserahmen (ORFs) organisiert ist, und anzunehmen, dass diese ORFs intakte HEV-Proteine kodieren.
- Eine unvollständige DNA-Sequenz des Genoms eines HEV-Stamms aus Burma (Myanmar) ist in Reyes et al., 1990, Science, 247: 1335–1339, offenbart. Tam et al., 1991, und Reyes et al., PCT-Patentanmeldung
WO 91/15603 - Ichikawa et al., 1991, Microbiol. Immunol., 35: 535–543, offenbaren die Isolierung einer Serie an Klonen mit einer Länge von 240–320 Nukleotiden durch das Screenen einer λgt11-Expressionsbibliothek mit Seren von HEV-infizierten Cynomolgus-Affen. Das von einem Klon exprimierte rekombinante Protein wurde in E. coli exprimiert. Dieses Fusionsprotein ist durch die 3'-Region des ORF-2 des Myanmar-Stamms von HEV kodiert.
- Die Expression von zusätzlichen Proteinen, die in der 3'-Region von ORF-2 eines mexikanischen Stamms von HEV und eines burmesischen Stamms von HEV kodiert sind, ist in Yarbough et al., 1991, J. Virology, 65: 5790–5797, beschrieben. Dieser Artikel beschreibt die Isolierung von zwei cDNA-Klonen, die von HEV abgeleitet sind. Diese Klone kodieren die Proteine in der 3'-Region von ORF-2. Die Klone wurden in E. coli als Fusionsproteine exprimiert.
- Purdy et al., 1992, Archives of Virology, 123: 335–349, und Favorov et al., 1992, J. of Medical Virology, 36: 246–250, offenbaren die Expression eines größeren ORF-2-Proteinfragments des Burma-Stamms in E. coli. Diese Referenzen sowie die vorher diskutierten offenbaren nur die Expression eines Teils des ORF-2-Gens unter Verwendung von bakteriellen Expressionssystemen. Erfolgreiche Expression des Volllängen-ORF-2-Proteins ist bis zur vorliegenden Erfindung nicht offenbart worden.
- In einem Vergleich ist die Genomorganisation und die morphologische Struktur von HEV am nächsten verwandt zu den Caliciviren. Von Interesse ist, dass die strukturellen Proteine der Caliciviren durch den 3'-Teil ihres Genoms kodiert sind (Neil, J. D. et al. (1991) J. Virol., 65: 5440–5447; und Carter, M. J. et al. (1992), J. Arch. Virol., 122: 223–235). Obwohl es keinen direkten Beweis gibt, dass der 3'-terminale Teil des HEV-Genoms auch die strukturellen Proteine kodiert, führte eine Expression von bestimmten kleinen Teilen der 3'-Genomregion in Bakterienzellen zu einer Produktion von Proteinen, die mit Anti-HEV-Seren in ELISA und in Western Blots reaktiv sind (Yarborough et al. (1991); Ichikawa et al. (1991); Favorov et al. (1992) und Dawson, G. J. et al. (1992) J. Virol. Meth., 38: 175–186). Jedoch war die Funktion eines ORF-2-Proteins als ein strukturelles Protein bis zur vorliegenden Erfindung nicht bewiesen.
-
WO 94/06913 WO 96/10580 -
WO 95/08632 -
WO 96/12807 - Die kleinen Proteine, die durch einen Teil des ORF-2-Gens kodiert werden, wurden in Immunoassays zum Nachweis von Antikörpern gegen HEV in Tierseren verwendet. Die Verwendung von kleinen bakteriell exprimierten Proteinen als Antigene in serologischen Immunoassays hat mehrere mögliche Nachteile. Zum ersten führt die Expression dieser kleinen Proteine in bakteriellen Zellen zu Löslichkeitsproblemen und unspezifischer Kreuzreaktivität von Patientenseren mit E. coli-Proteinen, wenn Rohlysate aus E. coli als Antigene in Immunoassays verwendet werden (Purdy et al. (1992)). Zum zweiten ist die Verwendung von Western Blots als einen ersten serologischen Test für Anti-HEV-Antikörper in Routine-Epidemiologie aufgrund der Zeit- und Kostenbeschränkungen unpraktisch. Ein ELISA unter Verwendung von kleinen Peptiden, die von dem 3'-terminalen Teil des HEV-Genoms abgeleitet sind, führte zum Nachweis von nur 41% Positiven bei Patienten, deren HEV-Infektion bekannt war. Zum dritten ist gezeigt worden, dass bei vielen Viren, einschließlich Picornavirdae, wichtige antigenische und immunogenische Epitope stark konformationsabhängig sind (Lemon, S. M. et al. (1991), in Hollinger, F. B., Lemon, S. M., Margolis, H. S. (Hrsg.): "Viral Hepatitis and Liver Disease", Williams und Wilkins, Baltimore, 20–24). Aus diesem Grund wird davon ausgegangen, dass eine Expression eines gesamten ORFs, das ein intaktes HEV-Gen kodiert, in einem eukaryotischen System zur Produktion eines Proteins führen würde, das HEV-Virus-ähnliche Partikel bilden könnte. Solch ein gesamtes ORF-Protein hätte eine immunologische Struktur, die näher zu der von (einem) nativen Capsidprotein(en) als die vorstehend genannten kleineren Proteine, die nur Teile der strukturellen Proteine von HEV darstellen, wäre. Daher würden diese gesamten ORF-Proteine wahrscheinlich als ein repräsentativeres Antigen und ein effizienteres Immunogen als die momentan verwendeten kleineren Proteine dienen.
- Zusammenfassung der Erfindung
- Die Erfindung betrifft ein DNA-Molekül mit einer Sequenz, die aus Nukleotiden besteht, die für ein Hepatitis E-Virus offenes Leseraster 2-Protein kodieren, wobei das Protein seinen Aminoterminus bei der Aminosäure 112 des offenen Leserasters 2 und seinen Carboxyterminus bei der Aminosäure 578 oder 607 des offenen Leserasters 2 hat, einen rekombinanten Expressionsvektor, der das DNA-Molekül umfasst, und eine Wirtszelle, die den Expressionsvektor enthält.
- Die Erfindung betrifft auch ein Verfahren zur Herstellung eines rekombinanten Hepatitis E-Virus offenes Leseraster 2-Proteins, wobei das Verfahren umfasst:
- (a) Kultivieren einer wie vorstehend beschriebenen Wirtszelle unter Bedingungen, die für eine Expression des Proteins geeignet sind, und
- (b) Gewinnen des exprimierten Proteins aus der Wirtszelle.
- Die Erfindung betrifft weiterhin ein Hepatitis E-Virus offenes Leseraster 2-Protein, das seinen Aminoterminus bei der Aminosäure 112 des offenen Leserasters 2 und seinen Carboxyterminus bei der Aminosäure 578 oder 607 des offenen Leserasters 2 hat, eine pharmazeutische Zusammensetzung, die das Protein und ein geeignetes Exzipienz, Verdünnungsmittel oder einen geeigneten Träger umfasst, die Verwendung des Proteins zur Herstellung eines Medikaments für eine Verwendung bei einer Vermeidung von Hepatitis E in einem Säuger, ein Vakzin für ein Immunisieren eines Säugers gegen Hepatitis E-Infektion, wobei das Vakzin das Protein in einem pharmazeutisch verträglichen Träger umfasst, und einen Kit zur Vermeidung von Hepatitis E in einem Säuger, wobei der Kit das Protein umfasst.
- Die Erfindung betrifft ferner ein Verfahren zum Nachweis von Antikörpern gegen Hepatitis E-Virus in einer biologischen Probe, wobei das Verfahren umfasst:
- (a) Kontaktieren der Probe mit einem Hepatitis E-Virus offenes Leseraster 2-Protein, das seinen Aminoterminus bei der Aminosäure 112 des offenen Leserasters 2 und seinem Carboxyterminus bei der Aminosäure 578 oder 607 des offenen Leserasters 2 hat, und
- (b) Nachweis von Immunkomplexen, die zwischen dem Protein und den Antikörpern gebildet werden, wobei ein Nachweis der Komplexe das Vorhandensein von Antikörpern gegen Hepatitis E-Virus in der Probe anzeigt.
- Die Erfindung betrifft auch einen Kit für eine Verwendung in einem Verfahren zum Nachweis von Antikörpern gegen Hepatitis E-Virus in einer biologischen Probe, wobei der Kit ein Hepatitis E-Virus offenes Leseraster 2-Protein umfasst, das seinen Aminoterminus bei der Aminosäure 112 des offenen Leserasters 2 und seinen Carboxyterminus bei der Aminosäure 578 oder 607 des offenen Leserasters 2 hat.
- Natürliche Nukleinsäuresequenzen, die fähig sind, die Produktion von HEV-Proteinen zu bestimmen, können von einer cDNA- oder genomischen Bibliothek isoliert werden, aus der das Gen, das fähig ist, eine Synthese der HEV-Proteine zu bestimmen, identifiziert und isoliert werden kann. Im Sinne der Anmeldung betrifft eine Nukleinsäuresequenz RNA, DNA, cDNA oder eine jegliche synthetische Variante davon, die für ein Protein kodiert.
- Verfahren zum Nachweis von Antikörpern, die spezifisch für Hepatitis E-Virus sind, in biologischen Proben sind nützlich zum Diagnostizieren einer Infektion und Krankheit, die durch HEV ausgelöst wird, und zum Überwachen des Verlaufs einer solchen Krankheit. Solche Verfahren sind auch nützlich zum Überwachen der Effizienz von therapeutischen Mitteln, während dem Verlauf einer Behandlung einer HEV-Infektion und -Krankheit in einem Säuger.
- Beschreibung der Abbildungen
-
1 zeigt den rekombinanten Vektor, der zur Expression des gesamten ORF-2-Proteins des Genoms des HEV-Stamms SAR-55 verwendet wurde. -
2A und2B sind Natriumdodecylsulfat-Polyacrylamidgele (SDS-PAGE), in denen Zell-Lysate von Insektenzellen, die mit Wildtyp-Baculovirus oder rekombinantem Baculovirus (der das ORF-2-kodierende Gen enthält) infiziert waren, entweder mit Coomassie-Blau (A) angefärbt waren oder einem Western-Blotting mit Serum eines HEV-infizierten Schimpansen unterworfen wurden (B). In sowohl2A als auch2B enthält Spur 1 Gesamt-Zell-Lysat von nicht-infizierten SF-9-Zellen, Spur 2 enthält Lysat von Zellen, die mit Wildtyp-Baculovirus infiziert worden waren, Spur 3 enthält Lysat von Zellen, die mit rekombinantem Baculovirus infiziert worden waren und Spur 4 enthält Molekulargewichtsmarker. -
3A und3B zeigen Immun-Elektronenmikroskopaufnahmen (IEM) von 30 bzw. 20 nm Virus-Like-Partikeln, die als Ergebnis der Expression von ORF-2-Protein in rekombinant infizierten Insektenzellen gebildet werden. -
4 zeigt die Ergebnisse eines ELISAs unter Verwendung von rekombinantem ORF-2, das von Insektenzellen exprimiert wurde, die das Gen enthalten, das den kompletten ORF-2 kodiert, als das Antigen. Serum-Anti-HEV-Antikörper-Niveaus wurden zu verschiedenen Zeitpunkten nach Inokulation von Cynomolgus-Affen mit entweder den mexikanischen (Cyno-80A82, Cyno-9A97 und Cyno 83) oder Pakistani-(Cyno-374) Stämmen von HEV bestimmt. -
5A –D zeigen die Ergebnisse eines ELISAs unter Verwendung von rekombinantem ORF-2, das von Insektenzellen exprimiert wurde, die das Gen enthalten, das das komplette ORF-2 kodiert, als das Antigen. Serum-IgG oder IgM-Anti-HEV-Niveaus wurden im Zeitverlauf nach Inokulation von zwei Schimpansen mit HEV bestimmt. -
6A –J zeigen einen Vergleich von ELISA-Daten, die unter Verwendung des rekombinanten kompletten ORF-2-Proteins, das von SAR-55 abgeleitet ist, als das Antigen bzw. eines rekombinanten partiellen ORF-2-Proteins, das von dem bur mesischen Stamm von HEV abgeleitet ist (Genelabs), als das Antigen erhalten wurden. -
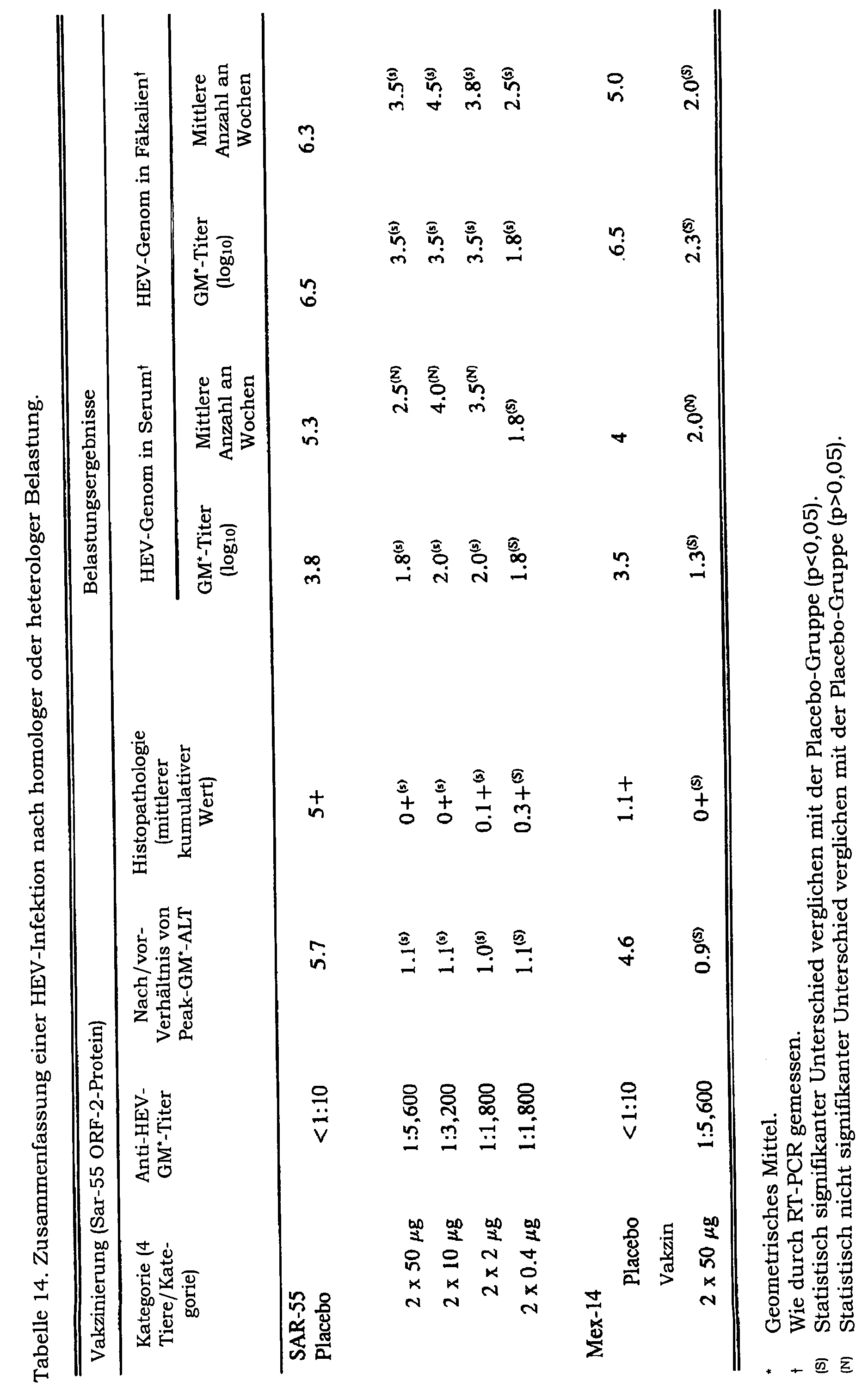
7A –J zeigen Anti-HEV-IgG-ELISA- und Alanin-Aminotransferase (ALT)-Werte für Cynomolgus-Affen, die mit 10-fachen seriellen Verdünnungen (angegeben in Klammern über jedem Schaubild) einer 10%igen fäkalen Suspension von SAR-55-HEV inokuliert waren. Rekombinante Antigene, die in ELISA verwendet wurden, waren: Glutathion-S-Transferase (GST); 3-2(M), eine Fusion des 3-2-Epitops [Yarbough et al., (1991) J. Virol., 65: 5790–5797] und GST; SG3 (B), eine Fusion von 327 C-terminalen Aminosäuren von ORF-2 und GST [Yarbough et al., (1993): Assay Development of Diagnostic Tests for Hepatitis E in "International Symposium an Viral Hepatitis and Liver Disease. Scientific Program and Abstract Volume." Tokyo:VHFL S. 87]; und ein 55 kDa ORF-2-Produkt, das direkt in Insektenzellen exprimiert wurde. -
8A –E zeigen Anti-HEV-IgM-ELISA- und ALT-Werte für positive Cynomolgus-Affen, die mit 10-fachen seriellen Verdünnungen (angegeben in Klammern über jedem Schaubild) der 10%igen fäkalen Suspension von SAR-55-HEV inokuliert waren. Rekombinante Antigene, die in ELISA verwendet wurden, waren: Glutathion-S-Transferase (GST); 3-2(M), eine Fusion des 3-2-Epitops [Yarbough et al., 1991] und (GST); SG3 (B), eine Fusion von 327 C-terminalen Aminosäuren von ORF-2 und GST [Yarbough et al., 1993]; und das 55 kDa ORF-2-Produkt, das direkt in Insektenzellen exprimiert wurde. -
9 zeigt eine Ethidiumbromid-Anfärbung eines 2%igen Agarosegels, auf dem PCR-Produkte getrennt wurden, die von Extrakten von seriellen 10-fachen Verdünnungen (angegeben über jeder Spur des Gels) der 10%igen fäkalen Suspension des SAR-55-HEV hergestellt wurden. Die vorhergesagte Länge der PCR-Produkte war etwa 640 Basenpaare und die mit einem (M) markierte Spalte enthält DNA-Größenmarker. -
10 zeigt den pPIC9-Vektor, der zur Expression des gesamten ORF-2-Proteins oder von Fragmenten mit geringerem Molekulargewicht in Hefe verwendet wurde. -
11 zeigt die schematische Organisation des Hepatitis E-Virus (HEV)-Genoms und von rekombinanten Baculoviren, die Volllängen-(bHEV ORF2 fl) und ver kürztes HEV-ORF2 (bHEV ORF2 5' tr und bHEV ORF2 5'-3' tr)-Capsidgene kodieren. -
12A und12B zeigen die zeitliche Proteinexpression von rekombinantem Baculovirus, der das HEV ORF2-Volllängengen kodiert. Sf-9-Insektenzellen wurden bei einer Multiplizität der Infektion (MOI) = 5 mit bHEV ORF2 fl-Virus infiziert. Infizierte Zellen und Medienüberstände wurden täglich während der viertägigen Infektion geerntet. Zell-Lysate und Medienüberstände wurden durch SDS-PAGE auf 8–16%igen Protein-Gradientengelen fraktioniert und mit kolloidalem Coomassie-Blau-Farbstoff angefärbt (12A ). Proteine von Duplikaten der Proteingele wurden auf Nitrocellulosemembranen durch Elektroblotten transferiert und HEV-Proteine wurden chromogen durch Antikörperbindung (12B ) an primäre Schimpansen-Antiseren gegen HEV (1:500) gefolgt von anti-humanes IgG2 – alkalische Phosphatase-Sekundärantiseren aus Ziege (1:5000) nachgewiesen. Spur 1, Sea-blue Molekulargewichtsmarker; Spur 2, scheininfizierte Zellen; Spur 3, Zellen ein Tag nach Infektion (p.i.); Spur 4, Zellen zwei Tage p.i.; Spur 5, Zellen drei Tage p.i.; Spur 6, Zellen vier Tage p.i.; Spur 7, Sea-blue Protein-Molekulargewichtsmarker; Spur 8, scheininfizierter Überstand; Spur 9, Überstand ein Tag p.i.; Spur 10, Überstand zwei Tage p.i.; Spur 11, Überstand drei Tage p.i.; Spur 12, Überstand vier Tage p.i. Die Zuordnungen der Spuren sind für Schaubilder A und B gleich. -
13A –13C zeigt Elutionsprofile einer Proteinchromatographie von Zell-Lysaten von mit bHEV ORF2 fl-Virus infizierten Insektenzellen.13A zeigt das Protein-Elutionsprofil einer Anionenaustauscherchromatographie auf einer Q-Sepharose Fast Flow starker Anionenaustauscher-Säule unter Verwendung eines linearen 0–300 mM NaCl-Gradienten in Q-Beladungspuffer.13B zeigt das Protein-Elutionsprofil des HEV-55 kD-Proteins von Peak-Q-Fraktionen auf einer SOURCE 15 Q-High-Performance-starker Anionenaustauscher-Säule unter Verwendung eines linearen 0–300 mM NaCl-Gradienten in Q-Beladungspuffer.13C zeigt das Elutionsprofil von zusammengeführten Fraktionen der SOURCE 15 Q-Chromatographie, die das 55 kDa-Protein enthielten und die dann einer Gelfiltration auf einer Sephacryl S 200-Säule unterworfen wurden. -
14 zeigt SDS-PAGE- und Western Blot-Ergebnisse des HEV-55 kD-Proteins, das in Gelfiltrationsfraktionen einer Sephacryl G 200-Säule enthalten war. Zusammengeführte Fraktionen, die das 55 kD-Protein der SOURCE 15 Q-Chromatographie von Zell-Lysaten enthielten, wurden einer Gelfiltration auf einer Seph acryl S-200-Säule unterworfen. Aliquots von ausgewählten Säulenfraktionen wurden SDS-PAGE- und Western Blot-Analysen (unteres Schaubild) oder einem mit Coomassie-Blau gefärbten 8–20%igen NOVEX-Gradientengel (oberes Schaubild) unterworfen. HEV-Proteine wurden durch Western Blot mit konvaleszenten Antiseren von HEV-infizierten Schimpansen nachgewiesen. Spur 1, Sea-blue Protein-Molekulargewichtsmarker; Spur 2, zusammengeführte Q-Fraktionen; Spuren 3–12, Gelfiltrationsfraktionen. -
15 zeigt das Peptidprofil eines Lys-C-Verdaus des rekombinanten HEV ORF2 55 kD-Proteins, das von Zell-Lysaten von Sf-9-Insektenzellen, die mit bHEV ORF2 fl-Virus infiziert waren, gereinigt wurde. -
16 zeigt die Ergebnisse einer carboxyterminalen Aminosäureanalyse von rekombinanten HEV ORF2 55 kD-Proteinen, die aus Zell-Lysaten von Sf-9-Insektenzellen, die mit bHEV ORF2 fl-Virus infiziert waren, gereinigt wurden. -
17 zeigt das Profil einer Elektronenspray-Massenspektroskopie des rekombinanten HEV 55 kD-Proteins, das aus Zell-Lysaten von Sf-9-Insektenzellen, die mit bHEV ORF2 fl-Virus infiziert waren, gereinigt wurde. -
18A und18B zeigen die zeitliche Proteinexpression von rekombinanten Baculoviren, die HEV ORF2-Gene kodieren. Sf-9-Insektenzellen wurden bei einer MOI = 5 mit bHEV ORF2 5' tr- oder 5'-3'-tr-Viren vier Tage p.i. infiziert. Infizierte Zellen und Medienüberstände wurden täglich während der viertägigen Infektion geerntet und wie in der Beschreibung zu12 beschrieben analysiert. -
18A und B zeigen SDS-PAGE-(Spuren 1–5) und Western Blot-(Spuren 6–10)-Ergebnisse von Zell-assoziierten Proteinen aus bHEV ORF2 5' tr-(18A ) bzw. 5'-3' tr-(18B )-Virusinfektionen.18C und D zeigen SDS-PAGE-(Spuren 1–5) und Western Blot-(Spuren 6–10)-Ergebnisse von sekretierten Proteinen aus bHEV ORF2-5' tr-(18C ) bzw. 5'-3' tr-18D )-Virusinfektionen. Spuren 1 und 6, scheininfizierte Zellen; Spuren 2 und 7, Zellen ein Tag p.i.; Spuren 3 und 8, Zellen zwei Tage p.i.; Spuren 4 und 9, Zellen drei Tage p.i.; und Spuren 5 und 10, Zellen vier Tage p.i. - Sea-blue Protein-Molekulargewichtsmarker wurden zur Bestimmung des Molekulargewichts von angegebenen Proteinen verwendet. Ein Anti-HEV-Antikörper aus mit lebendem HEV infizierten Schimpansen wurde zum Nachweis von HEV-Proteinen in Western Blots verwendet.
- Genaue Beschreibung der Erfindung
- Ein Pakistani-Stamm des Hepatitis E-Virus (HEV), SAR-55, ist isoliert und im Wesentlichen gereinigt worden. Die viralen Gene, die Proteine von HEV kodieren, sind kloniert worden und die rekombinanten Proteine sind unter Verwendung eines Expressionssystems exprimiert worden. Insbesondere sind die offenen Leserahmen (ORF) von HEV, die von SAR-55 abgeleitet sind, kloniert und exprimiert worden.
- HEV-Proteine sind isoliert worden. HEV-Proteine können im Wesentlichen homolog zu und am meisten bevorzugt biologisch äquivalent zu den nativen HEV-Proteinen sein. Mit "biologisch äquivalent" wie in der Beschreibung verwendet ist gemeint, dass die Zusammensetzungen antigen und/oder immunogen sind. Die HEV-Proteine können auch die Produktion von schützenden Antikörpern nach Injektion in einen Säuger stimulieren, die dazu dienen würden, den Säuger bei Belastung mit einem Wildtyp-HEV zu schützen. Mit "im Wesentlichen homolog" wie in der folgenden Beschreibung verwendet ist ein Grad an Homologie in der Aminosäuresequenz zu den nativen HEV-Proteinen gemeint. Vorzugsweise ist der Grad an Homologie größer als 70%, bevorzugt größer als 90%, mit einer besonders bevorzugten Gruppe an Proteinen, die mehr als 99% homolog zu den nativen HEV-Proteinen über den Bereich des Vergleichs zwischen den beiden Proteinen sind.
- Bevorzugte HEV-Proteine sind diejenigen Proteine, die durch die ORF-Gene kodiert werden. Von besonderem Interesse sind Proteine, die durch das ORF-2-Gen von HEV kodiert werden, und insbesondere Proteine, die durch das ORF-2-Gen des SAR-55-Stamms von HEV kodiert werden. Die Aminosäuresequenzen der ORF-1-, ORF-2- und ORF-3-Proteine sind nachstehend als SEQ ID NO: 1, SEQ ID NO: 2 bzw. SEQ ID NO: 3 gezeigt:
- Die Drei-Buchstaben-Abkürzungen entsprechen der herkömmlichen Aminosäure-Kurzschrift für die zwanzig natürlicherweise vorkommenden Aminosäuren.
- Die bevorzugten rekombinanten HEV-Proteine bestehen aus mindestens einem ORF-Protein. Andere rekombinante Proteine, die aus mehr als einem von demselben oder verschiedenen ORF-Proteinen hergestellt sind, können so hergestellt sein, dass sie die biologischen Eigenschaften des Proteins verändern. Es ist vorgesehen, dass Additionen, Substitutionen oder Deletionen von einzelnen Aminosäuren oder von einzelnen Sequenzen aus Aminosäuren die biologische Aktivität der HEV-Proteine erhöhen können.
- Eine Nukleinsäuresequenz, die fähig ist, die Produktion des vorstehend beschriebenen HEV-Proteins oder von Proteinen, die im Wesentlichen homolog zu den HEV-Proteinen sind, zu ermöglichen, bezeichnet als SAR-55, ist nachstehend als SEQ ID NO: 4 dargestellt und wurde bei der American Type Culture Collection (ATCC) am 17. September 1992 (ATCC-Zugangsnummer 75302) hinterlegt.
- Die für die Nukleotide verwendeten Abkürzungen sind die standardmäßig auf dem Fachgebiet verwendeten.
- Die Sequenz in eine Richtung ist wie herkömmlich als die "Plus"-Sequenz bezeichnet worden, da sie der Protein-kodierende Strang von RNA-Viren ist, und dies ist die vorstehend als SEQ ID NO: 4 gezeigte Sequenz.
- Die abgeleiteten Aminosäuresequenzen der offenen Leserahmen von SAR-55 haben SEQ ID NO: 1, SEQ ID NO: 2 und SEQ ID NO: 3. ORF-1 startet bei Nukleotid 28 von SEQ ID NO: 4 und erstreckt sich über 5078 Nukleotide; ORF-2 startet bei Nukleotid 5147 von SEQ ID NO: 4 und erstreckt sich über 1979 Nukleotide; und ORF-3 startet bei Nukleotid 5106 von SEQ ID NO: 4 und erstreckt sich über 368 Nukleotide.
- Variationen sind in der DNA-Sequenz vorgesehen, die zu einer DNA-Sequenz führen werden, die fähig ist, eine Produktion von Analogen des ORF-2-Proteins zu ermöglichen. Mit "Analoge des ORF-2-Proteins" wie in der Beschreibung verwendet ist ein Protein mit einer Aminosäuresequenz gemeint, die im Wesentlichen identisch zu einer Sequenz ist, die spezifisch hierin gezeigt ist, worin ein oder mehrere der Reste, die in den hierin gezeigten Sequenzen gezeigt sind, durch einen biologisch äquivalenten Rest ersetzt worden sind, so dass das resultierende Protein (d. h. das "Analog") antigen und/oder immunogen ist. Aufgrund der Degeneriertheit des genetischen Codes wird zu verstehen sein, dass eine Vielzahl an Auswahlen an Nukleotiden gemacht werden kann, die zu einer DNA-Sequenz führen, die fähig ist, eine Produktion der vorliegenden ORF-Proteine oder ihrer Analoga zu ermöglichen.
- Ein Verfahren zum Nachweis des Hepatitis E-Virus in biologischen Proben kann auf einer selektiven Amplifikation von Hepatitis E-Genfragmenten basieren. Vorzugsweise verwendet dieses Verfahren ein Paar einzelsträngiger Primer, die von nichthomologen Bereichen von entgegengesetzten Strängen eines DNA-Duplexfragments abgeleitet sind, das wiederum von einem Hepatitis E-Virus abgeleitet ist, dessen Genom einen Bereich enthält, der homolog zu der in SEQ ID NO: 4 gezeigten SAR-55-Sequenz ist. Diese Primer können in einem Verfahren verwendet werden, das dem Prozess einer Amplifizierung ausgewählter Nukleinsäuresequenzen wie in
US-Patent Nr. 4,683,202 definiert folgt. - Einzelsträngige Antisense-Poly- oder -Oligonukleotide, die von Sequenzen abgeleitet sind, die homolog zu der SAR-55-cDNA sind, können zur Hemmung der Expression von Hepatitis E-Genen verwendet werden. Diese Antisense-Poly- oder -Oligonukleo tide können entweder DNA oder RNA sein. Die Zielsequenz ist typischerweise Messenger-RNA und mehr bevorzugt eine Signalsequenz, die zur Prozessierung oder Translation der RNA benötigt wird. Die Antisense-Poly- oder Oligonukleotide können an ein Polykation wie ein Polylysin wie in Lemaitre, M. et al. (1989) Proc. Natl. Acad. Sci. USA 84: 648–652 offenbart konjugiert sein. Dieses Konjugat kann an einen Säuger in einer Menge verabreicht werden, die ausreichend ist, um an die Messenger-RNA zu hybridisieren und deren Funktion zu hemmen.
- Ein Verfahren mit rekombinanter DNA kann zur Herstellung von HEV-Proteinen, vorzugsweise einem Protein, das aus mindestens einem ORF-Protein, am meisten bevorzugt aus mindestens einem ORF-2-Protein besteht, verwendet werden. Das rekombinante ORF-Protein kann aus einem ORF-Protein oder einer Kombination aus dem gleichen oder verschiedenen ORF-Proteinen bestehen. Eine natürliche oder synthetische Nukleinsäuresequenz kann verwendet werden, um eine Produktion der HEV-Proteine zu ermöglichen. Das Verfahren kann umfassen:
- (a) Herstellen einer Nukleinsäuresequenz, die fähig ist, einem Wirtsorganismus zu ermöglichen, ein Protein von HEV zu produzieren;
- (b) Klonieren der Nukleinsäuresequenz in einen Vektor, der fähig ist, in einen Wirtsorganismus transferiert und darin repliziert zu werden, wobei ein solcher Vektor operable Elemente für die Nukleinsäuresequenz enthält;
- (c) Transferieren des Vektors, der die Nukleinsäure und operablen Elemente enthält, in einen Wirtsorganismus, der fähig, das Protein zu exprimieren;
- (d) Kultivieren des Wirtsorganismus unter Bedingungen, die für eine Amplifikation des Vektors und Expression des Proteins geeignet sind; und
- (e) Ernten des Proteins.
- Ein Verfahren für die rekombinante DNA-Synthese eines Proteins, das durch Nukleinsäuren von HEV, vorzugsweise einer Nukleinsäuresequenz, die mindestens ein ORF von HEV oder eine Kombination der gleichen oder unterschiedlicher ORF-Proteine kodiert, am meisten bevorzugt mindestens eine ORF-2-Aminosäuresequenz kodiert, kodiert wird, kann umfassen:
- (a) Kultivieren eines transformierten oder transfizierten Wirtsorganismus, der eine Nukleinsäuresequenz enthält, die fähig ist, dem Wirtsorganismus zu ermöglichen, ein Protein zu produzieren, unter Bedingungen, so dass das Protein produziert wird, wobei das Protein eine wesentliche Homologie zu einem nativen HEV-Protein (über dem Bereich des Vergleichs zwischen den beiden Proteinen), das von HEV isoliert wurde und die Aminosäuresequenz gemäß SEQ ID NO: 1, SEQ ID NO: 2 oder SEQ ID NO: 3 hat, aufweist, oder Kombinationen davon.
- Die RNA-Sequenz des viralen Genoms des HEV-Stamms SAR-55 kann wie folgt isoliert und zu cDNA kloniert werden. Virale RNA wird aus einer biologischen Probe extrahiert, die von mit SAR-55 infizierten Cynomolgus-Affen gesammelt wurde, und die virale RNA wird dann revers transkribiert und durch Polymerasekettenreaktion unter Verwendung von Primern amplifiziert, die komplementär zu dem Plus- oder Minus-Strang des Genoms eines HEV-Stamms aus Burma (Tam et al. (1991)) oder des SAR-55-Genoms sind. Die PCR-Fragmente werden in pBR322 oder pGEM-32 subkloniert und die doppelsträngigen PCR-Fragmente wurden sequenziert.
- Die für eine Verwendung in der vorliegenden Erfindung vorgesehenen Vektoren umfassen jegliche Vektoren, in die eine Nukleinsäuresequenz wie vorstehend beschrieben, zusammen mit jeglichen bevorzugten oder benötigten operablen Elementen, inseriert werden kann, wobei der Vektor dann nachfolgend in einen Wirtsorganismus transferiert und in einem solchen Organismus repliziert werden kann. Bevorzugte Vektoren sind diejenigen, deren Restriktionsstellen gut dokumentiert worden sind und die die operablen Elemente enthalten, die für eine Transkription der Nukleinsäuresequenz bevorzugt oder benötigt werden.
- Die "operablen Elemente" wie hierin beschrieben umfassen mindestens einen Promoter, mindestens ein Terminator-Codon und jegliche andere DNA-Sequenzen, die für eine geeignete Transkription und nachfolgende Translation der Vektornukleinsäure notwendig oder bevorzugt sind. Insbesondere ist vorgesehen, dass solche Vektoren mindestens einen Replikationsursprung, der von dem Wirtsorganismus erkannt wird, zusammen mit mindestens einem Selektionsmarker und mindestens einer Promotorsequenz, die fähig ist, eine Transkription der Nukleinsäuresequenz zu initiieren, enthalten werden.
- Bei der Konstruktion des erfindungsgemäßen Klonierungsvektors sollte zusätzlich beachtet werden, dass multiple Kopien der Nukleinsäuresequenz und ihrer zugehörigen operablen Elemente in jedem Vektor inseriert werden können. In solch einer Ausführungsform würde der Wirtsorganismus größere Mengen des erwünschten HEV-Proteins pro Vektor produzieren. Die Anzahl an multiplen Kopien der DNA-Sequenz (entweder eine einzelne Sequenz oder zwei verschiedene Sequenzen), die in den Vektor inseriert werden können, ist nur durch die Fähigkeit des resultierenden Vektors begrenzt, aufgrund seiner Größe in einem geeigneten Wirts-Mikroorganismus transferiert und in diesem repliziert und transkribiert zu werden.
- Restriktionsverdau-Fragmente, die eine kodierende Sequenz für HEV-Proteine enthalten, können in einem geeigneten Expressionsvektor, der in prokaryotischen oder eukaryotischen Zellen arbeitet, inseriert werden. Mit geeignet ist gemeint, dass der Vektor fähig ist, eine gesamte Nukleinsäuresequenz, die für HEV-Proteine, vorzugsweise mindestens ein ORF-Protein, kodiert, zu tragen und zu exprimieren. Bevorzugte Expressionsvektoren sind diejenigen, die in einer eukaryotischen Zelle arbeiten. Beispiele für solche Vektoren beinhalten in nicht begrenzender Weise Vektoren, die für eine Expression in Hefe (z. B. pPIC9-Vektor – Invitrogen) geeignet sind, Vacciniavirus-Vektoren, Adenovirus oder Herpesviren, vorzugsweise Baculovirus-Transfervektoren. Bevorzugte Vektoren sind p63-2, der das gesamte ORF-2-Gen enthält, und P59-4, der die gesamten ORF-3- und ORF-2-Gene enthält. Diese Vektoren wurden bei der American Type Culture Collection, 12301 Parklawn Drive, Rockville, MD 20852, USA am 10. September 1992 hinterlegt und haben die Zugangsnummern 75299 (P63-2) und 75300 (P59-4). Mehr bevorzugte Vektoren sind bHEV ORF-2 5' tr, der die Aminosäuren 112–660 von ORF-2 kodiert, bHEV ORF-2 5'-3' tr, der die Aminosäuren 112–607 von ORF-2 kodiert, und ein Baculovirus-Vektor, der die Aminosäuren 112–578 von HEV-ORF-2 kodiert. Beispiel 1 veranschaulicht das Klonieren des ORF-2-Gens in pBlueBac zur Herstellung von p63-2. Dieses Verfahren umfasst einen Verdau des Genoms des HEV-Stamms SAR-55 mit den Restriktionsenzymen NruI und BglII, Inserieren eines Polylinkers, der BlnI- und BglII-Stellen enthält, in die einzelne NheI-Stelle des Vektors und Inserieren des NruI-BglII-ORF-2-Fragments in BlnI-BglII-pBlueBac unter Verwendung eines Adapters.
- In einer Ausführungsform kann der ausgewählte rekombinante Expressionsvektor dann in ein geeignetes eukaryotisches Zellsystem für die Zwecke einer Expression des rekombinanten Proteins transfiziert werden. Solche eukaryotischen Zellsysteme umfassen in nicht begrenzender Weise Hefe und Zelllinien wie HeLa, MRC-5, CV-1, HuH7 oder HepG2. Ein bevorzugtes eukaryotisches Zellsystem sind Sf9-Insektenzellen. Ein bevorzugtes Verfahren umfasst die Verwendung der Baculovirus-Expressionsvektoren und der Insektenzelllinie Sf9.
- Das exprimierte rekombinante Protein kann durch bekannte Verfahren, die Coomassie-Blau-Färbung und Western-Blotting unter Verwendung von Seren, die Anti-HEV-Antikörper enthalten, wie in Beispiel 2 gezeigt, umfassen, nachgewiesen wer den. Ein anderes Verfahren ist der Nachweis von Virus-Like-Partikeln durch Immun-Elektronenmikroskopie wie in Beispiel 3 gezeigt.
- In einer weiteren Ausführungsform kann das durch die Sf9-Zellen exprimierte rekombinante Protein als ein Rohlysat erhalten werden oder es kann durch bekannte Standard-Proteinreinigungsverfahren, die differenzielle Präzipitation, Molekularsieb-Chromatographie, Ionenaustauschchromatographie, isoelektrische Fokussierung, Gelelektrophorese, Affinitäts- und Immunaffinitätschromatographie und dergleichen umfassen können, gereinigt werden. Im Falle der Immunaffinitätschromatographie kann das rekombinante Protein durch Durchfluss durch eine Säule gereinigt werden, die ein Harz enthält, an das Antikörper gebunden sind, die für das ORF-Protein spezifisch sind. Ein Beispiel für Protokolle zur Reinigung eines rekombinant exprimierten HEV-ORF-2-Proteins aus geklärten Lysaten von Baculovirusinfizierten Zellen bzw. Medienüberständen ist in Beispiel 16 beschrieben.
- In einer anderen Ausführungsform können die exprimierten rekombinanten erfindungsgemäßen Proteine in Immunoassays zur Diagnose oder Prognose von Hepatitis E in einem Säuger, der in nicht begrenzender Weise Menschen, Schimpansen, Altweltaffen, Neuweltaffen, andere Primaten und dergleichen umfasst, verwendet werden. In einer bevorzugten Ausführungsform ist der Immunoassay für eine Diagnose einer Hepatitis E-Infektion in Menschen geeignet. Immunoassays, die die HEV-Proteine, insbesondere die ORF-Proteine und besonders ORF-2-Proteine verwenden, stellen im Gegensatz zu Immunoassays, die partielle ORF-Proteine verwenden, ein hoch spezifisches, sensitives und reproduzierbares Verfahren zur Diagnose von HEV-Infektionen bereit.
- Erfindungsgemäße Immunoassays können ein Radioimmunoassay, Western Blot-Assay, Immunfluoreszenzassay, Enzym-Immunoassay, Chemilumineszenzassay, immunohistochemischer Assay und dergleichen sein. Bekannte Standard-Techniken für ELISA sind in Methods in Immunodiagnosis, 2. Ausgabe, Rose und Bigazzi, Hrsg., John Wiley and Sons, 1980, und Campbell et al., Methods of Immunology, W. A. Benjamin, Inc., 1964, beschrieben, die beide hierin durch Bezugnahme eingebunden sind. Solche Assays können ein direkter, indirekter, kompetitiver oder nicht-kompetitiver Immunoassay wie im Fachgebiet beschrieben sein (Oellerich, M., 1984, J. Clin. Chem. Clin. Biochem. 22: 895–904). Für solche Nachweisassays geeignete biologische Proben umfassen in nicht begrenzender Weise Gewebebiopsieex trakte, Gesamtblut, Plasma, Serum, Cerebrospinalflüssigkeit, Pleuralflüssigkeit, Urin und dergleichen.
- Testserum kann mit einem Festphasenreagenz mit einem Oberflächen-gebundenen rekombinanten HEV-Protein als ein Antigen, vorzugsweise einem ORF-Protein oder einer Kombination aus unterschiedlichen ORF-Proteinen wie ORF-2 und ORF-3, ORF-1 und ORF-3 und dergleichen, reagiert werden. Am meisten bevorzugt ist das HEV-Protein ein Protein, das im Wesentlichen aus Aminosäuren 112–607 von HEV-ORF-2 besteht. Das Reagenz mit fester Oberfläche kann durch bekannte Techniken zum Anbringen eines Proteins an Festträgermaterial hergestellt werden. Diese Anbringungsverfahren umfassen unspezifische Adsorption des Proteins an den Träger oder kovalente Anbringung des Proteins an eine reaktive Gruppe auf dem Träger. Nach Reaktion des Antigens mit Anti-HEV-Antikörper werden ungebundene Serum-Komponenten durch Waschen entfernt und der Antigen-Antikörper-Komplex wird mit einem Zweitantikörper wie einem markierten Anti-Mensch-Antikörper reagiert. Die Markierung kann ein Enzym sein, dass durch Inkubation des Festträgers in Anwesenheit eines geeigneten fluorimetrischen oder kolorimetrischen Reagenzes nachgewiesen wird. Andere nachweisbare Markierungen wie Radiomarkierungen oder kolloidales Gold und dergleichen können auch verwendet werden.
- In einer bevorzugten Ausführungsform wird das Protein, das durch den rekombinanten Baculovirus-Vektor exprimiert wird, der die ORF-2-Sequenz von SAR-55 enthält, die für Aminosäuren 112–607 von HEV-ORF-2 kodiert, als ein spezifischer Bindewirkstoff zum Nachweis von Anti-HEV-Antikörpern, vorzugsweise IgG- oder IgM-Antikörpern verwendet. Beispiel 10 zeigt die Ergebnisse eines ELISAs, bei dem das Festphasenreagenz das rekombinante 55 kDa-Protein, das aus Aminosäuren 112–607 besteht, als das Oberflächenantigen aufweist. Dieses Protein ist fähig, Antikörper nachzuweisen, die als Antwort auf verschiedene Stämme von HEV produziert wurden, aber es weist keine Antikörper nach, die als Antwort auf Hepatitis A, B, C oder D produziert wurden.
- Das HEV-Protein und Analoga können in Form eines Kits, alleine oder in Kombinationen mit anderen Reagenzien wie Zweitantikörpern, zur Verwendung in Immunoassays hergestellt werden.
- Die rekombinanten HEV-Proteine, vorzugsweise ein ORF-Protein oder eine Kombination von ORF-Proteinen, mehr bevorzugt ein ORF-2-Protein und im Wesentlichen homologe Proteine und Analoga, können als ein Vakzin zum Schutz von Säugern gegen eine Belastung mit Hepatitis E verwendet werden. Das Vakzin, das als ein Immunogen wirkt, kann eine Zelle, ein Zell-Lysat von Zellen, die mit einem rekombinanten Expressionsvektor transfiziert sind, oder ein Kulturüberstand, der das exprimierte Protein enthält, sein. Alternativ ist das Immunogen ein teilweise oder im Wesentlichen gereinigtes rekombinantes Protein. Während es für das Immunogen möglich ist, in einer reinen oder im Wesentlichen reinen Form verabreicht zu werden, ist es bevorzugt, dass es in einer pharmazeutischen Zusammensetzung, Formulierung oder Zubereitung vorliegt.
- Formulierungen sowohl für eine veterinäre als auch eine humane Verwendung können ein Immunogen wie vorstehend beschrieben zusammen mit einem oder mehreren pharmazeutisch verträglichen Trägern und gegebenenfalls anderen therapeutischen Inhaltsstoffen beinhalten. Der/die Träger muss/müssen "verträglich" im Sinne von kompatibel mit den anderen Inhaltsstoffen der Formulierung und nicht schädlich für den Empfänger davon sein. Die Formulierungen können herkömmlicherweise in Einheitsdosisform vorliegen und können durch ein jegliches in der pharmazeutischen Technik bekanntes Verfahren hergestellt werden.
- Alle Verfahren umfassen den Schritt des Zusammenbringens des Wirkstoffs mit dem Träger, der einen oder mehrere Hilfsstoffe umfasst. Im Allgemeinen werden die Formulierungen durch einheitliches und direktes Zusammenbringen des Wirkstoffs mit flüssigen Trägern oder fein aufgespalteten festen Trägern oder beidem und dann, falls notwendig, Formen des Produkts in die erwünschte Formulierung hergestellt.
- Formulierungen, die für eine intravenöse, intramuskuläre, subkutane oder intraperitoneale Verabreichung geeignet sind, umfassen gewöhnlich sterile wässrige Lösungen des Wirkstoffs mit Lösungen, die bevorzugt isotonisch mit dem Blut des Empfängers sind. Solche Formulierungen können gewöhnlich durch Lösen eines festen Wirkstoffs in Wasser, das physiologisch kompatible Substanzen wie Natriumchlorid (z. B. 0,1–2,0 M), Glycin und dergleichen enthält und einen gepufferten pH-Wert aufweist, der mit physiologischen Bedingungen kompatibel ist, zur Herstellung einer wässrigen Lösung und Sterilisieren der Lösung hergestellt werden. Diese können in Einheits- oder Multidosis-Behältern, z. B. verschlossenen Ampullen oder Fläschchen, vorhanden sein.
- Die erfindungsgemäßen Formulierungen können einen Stabilisator umfassen. Beispielhafte Stabilisatoren sind Polyethylenglykol, Proteine, Saccharide, Aminosäuren, anorganischen Säuren und organische Säuren, die entweder alleine oder als Gemische verwendet werden können. Diese Stabilisatoren sind vorzugsweise in einer Menge von 0,11–10000 Gewichtsanteilen pro Gewichtsanteil immunogen eingebaut. Wenn zwei oder mehr Stabilisatoren verwendet werden sollen, liegt ihre Gesamtmenge vorzugsweise innerhalb des vorstehend angegebenen Bereichs. Diese Stabilisatoren werden in wässrigen Lösungen bei der geeigneten Konzentration und dem geeigneten pH-Wert verwendet. Der spezifische osmotische Druck solcher wässrigen Lösungen ist im Allgemeinen im Bereich von 0,1–3,0 Osmol, vorzugsweise im Bereich von 0,8–1,2. Der pH-Wert der wässrigen Lösung ist innerhalb des Bereichs von 5,0–9,0, vorzugsweise innerhalb des Bereichs von 6–8 eingestellt. Beim Formulieren des erfindungsgemäßen Immunogens können Anti-Adsorptionsmittel verwendet werden.
- Zusätzliche pharmazeutische Verfahren können zur Steuerung der Wirkdauer verwendet werden. Zubereitungen für eine gesteuerte Abgabe können durch die Verwendung von Polymer zum Komplexieren oder Absorbieren der Proteine oder ihrer Derivate erhalten werden. Die gesteuerte Zufuhr kann durch Auswählen geeigneter Makromoleküle (z. B. Polyester, Polyaminosäuren, Polyvinyl, Pyrrolidon, Ethylenvinylacetat, Methylcellulose, Carboxymethylcellulose oder Protaminsulfat) und der Konzentration von Makromolekülen sowie der Verfahren zum Einbau ausgeführt werden, um eine Abgabe zu steuern. Ein anderes mögliches Verfahren zum Steuern der Wirkdauer durch Zubereitungen für eine gesteuerte Abgabe ist das Einbauen der Proteine, Proteinanaloga oder ihrer funktionellen Derivate in Partikel eines polymeren Materials wie Polyester, Polyaminosäuren, Hydrogele, Polymilchsäure) oder Ethylenvinylacetat-Copolymere. Anstatt dem Einbau dieser Mittel in polymere Partikel ist es alternativ möglich, diese Materialien in Mikrokapseln, die z. B. durch Co-Adservierungstechniken oder durch Grenzflächenpolymerisation hergestellt wurden, z. B. Hydroxymethylcellulose- oder Gelatine-Mikrokapseln bzw. Poly(methylmethacrylat)-Mikrokapseln, oder in kolloidale Arzneimittelzufuhrsysteme, z. B. Liposomen, Albumin-Mikrosphären, Mikroemulsionen, Nanopartikel und Nanokapseln, oder in Makroemulsionen einzuschließen.
- Wenn orale Zubereitungen erwünscht sind, können die Zusammensetzungen mit typischen Trägern wie unter anderem Laktose, Sucrose, Stärke, Talkum, Magne siumstearat, kristalline Cellulose, Methylcellulose, Carboxymethylcellulose, Glycerin, Natriumalginat oder Gummi arabicum kombiniert werden.
- Die erfindungsgemäßen Proteine können in der Form eines Kits, alleine oder in der Form einer pharmazeutischen Zusammensetzung wie vorstehend beschrieben bereitgestellt werden.
- Vakzinierung kann durch herkömmliche Verfahren ausgeführt werden. Zum Beispiel kann das Immunogen in einem geeigneten Verbindungsmittel wie Kochsalzlösung oder Wasser oder in vollständigen oder unvollständigen Adjuvanzien verwendet werden. Des Weiteren kann das Immunogen an einen Träger gebunden sein, um das Protein immunogen zu machen. Beispiele für solche Trägermoleküle umfassen in nicht begrenzender Weise Rinderserumalbumin (BSA), Keyhole-Limpet-Hämocyanin (KLH), Tetanustoxoid und dergleichen. Das Immunogen kann durch einen jeglichen Weg, der für eine Antikörperproduktion geeignet ist, wie intravenös, intraperitoneal, intramuskulär, subkutan und dergleichen, verabreicht werden. Das Immunogen kann einmalig oder bei periodischen Intervallen verabreicht werden, bis ein signifikanter Titer an Anti-HEV-Antikörper produziert wird. Der Antikörper kann in Serum unter Verwendung eines Immunoassays nachgewiesen werden.
- Ein Immunogen kann eine Nukleinsäuresequenz sein, die fähig ist, eine Synthese eines HEV-ORF-Proteins in einem Wirtsorganismus zu ermöglichen. Eine solche Nukleinsäuresequenz kann in einem geeigneten Expressionsvektor durch dem Fachmann bekannte Verfahren inseriert werden. Expressionsvektoren, die zum Erreichen eines hocheffizienten Gentransfers in vivo geeignet sind, umfassen in nicht begrenzender Weise retrovirale, adenovirale und Vaccinia-virale Vektoren. Operable Elemente solcher Expressionsvektoren sind vorstehend in dieser Beschreibung offenbart und dem Fachmann bekannt. Solche Expressionsvektoren können intravenös, intramuskulär, subkutan, intraperitoneal oder oral verabreicht werden.
- Direkter Gentransfer kann durch intramuskuläre Injektion von z. B. Plasmid-basierten eukaryotischen Expressionsvektoren, die eine Nukleinsäuresequenz enthalten, die fähig ist, eine Synthese von HEV-ORF-Protein(en) in einem Wirtsorganismus zu ermöglichen, erreicht werden. Ein solcher Ansatz ist bereits zur Herstellung des Hepatitis B-Oberflächenantigens in vivo verwendet worden und führte zu einer Antikörper-Antwort gegen das Oberflächenartigen (Davis, H. L. et al. (1993) Human Molecular Genetics, 2: 1847–1851; siehe auch Davis et al. (1993) Human Gene Thera py, 4: 151–159 und 733–740; und Davis, H. L. et al., Proc. Natl. Acad. Sci. USA (1996) 93: 7213–7218).
- Wenn das Immunogen ein teilweise oder im Wesentlichen gereinigtes rekombinantes HEV-ORF-Protein ist, reichen Dosen, die wirksam sind, eine schützende Antikörper-Antwort gegen HEV hervorzurufen, von etwa 0,1 µg bis etwa 100 µg. Ein mehr bevorzugter Bereich ist von etwa 0,5 µg bis etwa 70 µg und ein am meisten bevorzugter Bereich ist von etwa 10 µg bis etwa 50 µg.
- Dosen an HEV-ORF-Protein-kodierender Nukleinsäuresequenz, die wirksam ist, eine schützende Antikörper-Antwort gegen HEV hervorzurufen, reichen von etwa 1 bis etwa 5000 µg. Ein mehr bevorzugter Bereich ist etwa 300 bis etwa 2000 µg.
- Die Expressionsvektoren, die eine Nukleinsäuresequenz enthalten, die fähig ist, eine Synthese von HEV-ORF-Protein(en) in einem Wirtsorganismus zu ermöglichen, können in der Form eines Kits, alleine oder in der Form einer pharmazeutischen Zusammensetzung wie vorstehend beschrieben bereitgestellt werden.
- Die Verabreichung des erfindungsgemäßen Immunogens kann entweder für einen prophylaktischen oder für einen therapeutischen Zweck erfolgen. Wenn es prophylaktisch gegeben wird, wird das Immunogen vor einer jeglichen Belastung mit HEV oder vor einem jeglichen Symptom aufgrund einer HEV-Infektion gegeben. Die prophylaktische Verabreichung des Immunogens dient zur Verhinderung oder Abmilderung einer jeglichen nachfolgenden Infektion mit HEV in einem Säuger. Wenn es therapeutisch gegeben wird, wird das Immunogen bei (oder kurz nach) dem Beginn der Infektion oder bei dem Beginn eines jeglichen Symptoms einer Infektion oder Krankheit, die durch HEV verursacht wird, gegeben. Die therapeutische Verabreichung des Immunogens dient der Abschwächung der Infektion oder Krankheit.
- Ein Vakzin kann unter Verwendung eines rekombinanten ORF-2-Proteins, das durch die ORF-2-Sequenz des HEV-Stamms SAR-55 exprimiert wird, und von Äquivalenten davon hergestellt werden. Da gezeigt wurde, dass das rekombinante ORF-2-Protein Schutz gegen Belastung mit heterologen oder homologen HEV-Stämmen bietet, ist ihr Nutzen beim Schutz gegen eine Vielzahl an HEV-Stämmen angezeigt.
- Zusätzlich zur Verwendung als ein Vakzin können die Zusammensetzungen zur Herstellung von Antikörpern gegen HEV-Virus-Like-Partikel verwendet werden. Die Antikörper können direkt als antivirale Mittel verwendet werden. Zur Herstellung von Antikörpern wird ein Wirtstier unter Verwendung der Viruspartikel immunisiert oder, soweit angemessen, werden Nicht-Partikel-Antigene, die in dem Viruspartikel vorkommen, wie vorstehend für Vakzine beschrieben an einen Träger gebunden. Das Wirtsserum oder -plasma wird nach einem angemessenen Zeitintervall gesammelt, um eine Zusammensetzung bereitzustellen, die Antikörper umfasst, die mit dem Viruspartikel reagieren. Die Gamma-Globulin-Fraktion oder die IgG-Antikörper können z. B. durch Verwendung von gesättigtem Ammoniumsulfat oder DEAE-Sephadex oder anderen dem Fachmann bekannte Techniken erhalten werden. Die Antikörper sind im Wesentlichen frei von vielen der Nebenwirkungen, die mit anderen anti-viralen Mitteln wie Arzneimitteln assoziiert sein können.
- Die Antikörperzusammensetzungen können durch Minimierung möglicher ungünstiger Immunsystemantworten sogar noch kompatibler mit dem Wirtssystem gemacht werden. Dies wird durch Entfernung des gesamten oder eines Teils des Fc-Teils eines Antikörpers einer fremden Spezies oder Verwendung eines Antikörpers derselben Spezies wie das Wirtstier, z. B. die Verwendung von Antikörpern aus Mensch/menschlichem Hybridom, erreicht. Humanisierte Antikörper (d. h. nicht immunogen in einem Menschen) können z. B. durch Ersetzen eines immunogenen Teils eines Antikörpers durch einen entsprechenden, jedoch nicht immunogenen Teil (d. h. chimäre Antikörper) hergestellt werden. Solche chimären Antikörper können den reaktiven oder Antigen-bindenden Teil eines Antikörpers von einer Spezies und den Fc-Teil eines Antikörpers (nicht immunogen) von einer anderen Spezies enthalten. Beispiele von chimären Antikörpern umfassen in nicht begrenzender Weise nicht-menschliche Säuger-Mensch-Chimäre, Nager-Mensch-Chimäre, Maus-Mensch- und Ratte-Mensch-Chimäre (Robinson et al., internationale Patentanmeldung 184,187; Taniguchi M.,
europäische Patentanmeldung 171,496 europäische Patentanmeldung 173,494 WO 86/01533 - Allgemeine Überblicke über "humanisierte" chimäre Antikörper werden durch Morrison S., 1985, Science 229: 1202 und durch Oi et al., 1986, BioTechniques 4: 214 bereitgestellt.
- Geeignete "humanisierte" Antikörper können alternativ durch CDR- oder CEA-Substitution hergestellt werden (Jones et al., 1986, Nature 321: 552; Verhoeyan et al., 1988, Science 239: 1534; Biedler et al., 1988, J. Immunol. 141: 4053, die alle hierein durch Bezugnahme eingeschlossen sind).
- Die Antikörper oder Antigen-bindenden Fragmente können auch durch Gentechnik hergestellt werden. Die Technologie zur Expression von sowohl schwere als auch leichte Ketten-Genen in E. coli ist der Gegenstand der PCT-Patentanmeldungen mit den Veröffentlichungsnummern
WO 901443 WO 901443 WO 9014424 - Die Antikörper können auch als ein Mittel zum Erhöhen der Immunantwort verwendet werden. Die Antikörper können in Mengen verabreicht werden, die ähnlich zu denjenigen sind, die für andere therapeutische Verabreichungen von Antikörpern verwendet werden. Zum Beispiel wird zusammengeführtes Gamma-Globulin bei 0,02–0,1 ml/1b Körpergewicht während der frühen Inkubationsperiode anderer viraler Erkrankungen wie Tollwut, Masern und Hepatitis B zum Stören des viralen Eintritts in Zellen verabreicht. Daher können Antikörper, die mit den HEV-Viruspartikeln reagieren, alleine oder in Verbindung mit einem anderen anti-viralen Mittel an einen Wirt, der mit einem HEV infiziert ist, zur Erhöhung der Wirksamkeit eines antiviralen Arzneimittels passiv verabreicht werden.
- Alternativ können Anti-HEV-Antikörper durch Verabreichung von anti-idiotypen Antikörpern als Immunogene induziert werden. Herkömmlicherweise wird eine gereinigte Anti-HEV-Antikörperpräparation, die wie vorstehend beschrieben hergestellt wurde, zum Induzieren eines anti-idiotypen Antikörpers in einem Wirtstier verwendet. Die Zusammensetzung wird an das Wirtstier in einem geeigneten Verdünnungsmittel verabreicht. Nach Verabreichung, gewöhnlich wiederholter Verabreichung, produziert der Wirt einen anti-idiotypen Antikörper. Um eine immunogene Antwort gegen die Fc-Region zu beseitigen, können Antikörper verwendet werden, die durch dieselbe Spezies wie das Wirtstier hergestellt wurden, oder die Fc-Region der verabreichten Antikörper kann entfernt werden. Nach Induktion eines anti-idiotypen Antikörpers in dem Wirtstier wird Serum oder Plasma zur Bereitstellung einer Antikörperzusammensetzung entfernt. Die Zusammensetzung kann wie vorstehend für Anti-HEV-Antikörper beschrieben oder durch Affinitätschromatographie unter Verwendung von Anti-HEV-Antikörpern, die an die Affinitätsmatrix gebunden sind, gereinigt werden. Die hergestellten anti-idiotypen Antikörper sind in der Konformation ähnlich zu dem authentischen HEV-Antigen und können anstatt der Verwendung eines HEV-Partikelantigens zur Herstellung eines HEV-Vakzins verwendet werden.
- Wenn sie als Mittel zum Induzieren von Antivirus-Antikörpern in einem Tier verwendet werden, ist die Art und Weise der Injektion des Antikörpers die gleiche wie für Vakzinierungszwecke, d. h. intramuskulär, intraperitoneal, subkutan oder dergleichen in einer wirksamen Konzentration in einem physiologisch geeigneten Verdünnungsmittel mit oder ohne Adjuvanz. Eine oder mehrere Auffrischinjektionen können wünschenswert sein.
- Die erfindungsgemäßen HEV-abgeleiteten Proteine sind auch für eine Verwendung zur Herstellung von Antiserum, das für eine Prophylaxe vor oder nach einer Belastung konzipiert ist, vorgesehen. Hierbei wird ein HEV-Protein oder ein Gemisch an Proteinen mit einem geeigneten Adjuvanz formuliert und durch Injektion an menschliche Freiwillige gemäß bekannter Verfahren zur Herstellung humaner Antiseren verabreicht. Eine Antikörperantwort gegen die injizierten Proteine wird während einer Zeitspanne von mehreren Wochen nach Immunisierung durch periodische Serumprobenentnahme zum Nachweis der Anwesenheit von Anti-HEV-Serumantikörpern unter Verwendung eines Immunoassays wie hierin beschrieben überwacht.
- Das Antiserum von immunisierten Individuen kann als eine prophylaktische Maßnahme vor einer Belastung für Individuen, die einem Risiko ausgesetzt sind, sich eine Infektion zuzuziehen, verabreicht werden. Das Antiserum ist auch für eine Behandlung eines Individuums nach Belastung analog zur Verwendung von Hochtiter-Antiserum gegen Hepatitis B-Virus für eine Prophylaxe nach Belastung geeignet. Natürlich würde der Fachmann leicht verstehen, dass Immunglobulin (HEV-Immunglobulin), das von dem Antiserum von immunisierten Individuen unter Verwendung von Standardtechniken gereinigt wurde, als eine prophylaktische Maßnahme vor einer Belastung oder bei einer Behandlung von Individuen nach einer Belastung verwendet werden kann.
- Für sowohl in vivo-Verwendungen von Antikörpern gegen HEV-Virus-Like-Partikel und Proteine und anti-idiotype Antikörper als auch diagnostische Verwendung kann es bevorzugt sein, monoklonale Antikörper zu verwenden. Monoklonale Anti-Viruspartikel-Antikörper oder Anti-Idiotyp-Antikörper können wie folgt hergestellt werden. Die Milzzellen oder Lymphozyten eines immunisierten Tiers werden entfernt und immortalisiert oder zur Herstellung von Hybridomen durch dem Fachmann bekannte Verfahren verwendet. (Goding, J. W., 1983, Monoclonal Antibodies: Principles and Practice, Pladermic Press, Inc., NY, NY, Seiten 56–97). Zur Herstellung eines Mensch-Mensch-Hybridoms wird ein menschlicher Lymphozytenspender ausgewählt. Ein Spender, von dem bekannt ist, dass er mit HEV infiziert ist (wobei Infektion z. B. durch die Anwesenheit von Anti-Virus-Antikörpern im Blut oder durch eine Viruskultur gezeigt worden ist), kann als ein geeigneter Lymphozytenspender dienen. Lymphozyten können aus einer Probe von peripherem Blut isoliert werden oder Milzzellen können verwendet werden, wenn der Spender einer Milzentfernung unterzogen wird. Epstein-Barr-Virus (EBV) kann zur Immortalisierung menschlicher Lymphozyten verwendet werden oder ein menschlicher Fusionspartner kann zur Herstellung von Mensch-Mensch-Hybridomen verwendet werden. Primäre in vitro-Immunisierung mit Peptiden kann auch bei der Herstellung von humanen monoklonalen Antikörpern verwendet werden.
- Antikörper, die durch die immortalisierten Zellen sekretiert werden, werden zur Bestimmung der Klone gescreent, die Antikörper der gewünschten Spezifität sekretieren. Für monoklonale Anti-Viruspartikel-Antikörper müssen die Antikörper an HEV-Viruspartikel binden. Für monoklonale Anti-Idiotyp-Antikörper müssen die Antikörper an Anti-Viruspartikel-Antikörper binden. Zellen, die Antikörper der gewünschten Spezifität produzieren, werden ausgewählt.
- In einer anderen Ausführungsform werden monoklonale Antikörper durch Ernten von Messenger-RNA, die V-Gene von B-Zellen kodiert, von Menschen oder Schimpansen, die gegen das Antigen von Interesse immun sind, abgeleitet. Die Messenger-RNAs, die die leichten und schweren Ketten von Immunoglobulinen kodieren, werden durch reverse Transkriptase-Polymerasekettenreaktion amplifiziert, zufällig kombiniert und in filamentöse Phagen für einen Display kloniert. Die Phagen werden dann auf das Tragen von Antikörpern von Interesse durch "panning" über das Antigen der Wahl, das an eine Festphase angebracht ist, selektiert. Die wieder gewonnenen Phagen, die die Kombinationsstellen von Antikörpern aufweisen, die homolog zu dem Antigen sind, werden amplifiziert und die von ihnen getragenen Antikörpergene werden zusammengesetzt, um komplette Antikörpermoleküle zu kodieren. Solche Antikörper, die für das Antigen von Interesse spezifisch sind, werden in E. coli exprimiert, gereinigt und wie vorstehend für humane monoklonale Antikörper beschrieben verwendet. Herstellung von humanen monoklonalen Antikörpern aus kombinatorischen Bibliotheken wird zum Beispiel in Hoogenboom, H. R., und Winter, G., (1992) Journal of Molecular Biology, Band 227, Seiten 381–388, und in Chanock, R. M., et al., (1993) Infectious Agents and Disease, Band 2, Seiten 118–131 beschrieben.
- Die vorstehend beschriebenen Antikörper und Antigen-bindenden Fragmente davon können in Form eines Kits, alleine oder als eine pharmazeutische Zusammensetzung für eine in vivo-Verwendung bereitgestellt werden. Die Antikörper können für therapeutische Verwendungen, eine diagnostische Verwendung in Immunoassays oder als ein Immunaffinitätsmittel zur Reinigung von ORF-Proteinen wie hierin beschrieben verwendet werden.
- Material
- Die in den Beispielen verwendeten Materialien waren die folgenden: Primaten. Schimpanse (Chimp) (Pan troglodytes). Altweltaffen: Cynomolgus-Affen (Cyno) (Macaca fascicularis), Rhesusaffen (Rhesus) (M. mulatta), Schweinsaffen (PT) (M. nemestrina), und grüne Meerkatzen (AGM) (Cercopithecus aethiops). Neuweltaffen: Schnurrbarttamarine (Tam) (Saguinus mystax), Totenkopfaffen (SQM) (Saimiri sciureus) und Nachtaffen (OWL) (Aotus trivigatus). Primaten wurden einzeln unter Bedingungen zur Eingrenzung biologischer Gefährdung gehalten. Der Käfig, die Haltung und die Pflege der Tiere erfüllten alle Erfordernisse der Primatenhaltung oder übertrafen diese.
- Die meisten Tiere wurden intravenös mit HEV, Stamm SAR-55, das in 0,5 ml einer Stuhlsuspension, die mit fötalem Kälberserum verdünnt wurde, wie in Tsarev, S. A. et al. (1992), Proc. Natl. Acad. Sci. USA, 89: 559–563 und Tsarev, S. A. et al. (1993), J. Infect. Dis. (167: 1302–1306) beschrieben inokuliert.
- Chimp-1313 und 1310 wurden mit einer Vereinigung von Stuhlmaterialien, die von sieben Pakistani-Hepatitis E-Patienten gesammelt wurden, inokuliert.
- Serumproben wurden etwa zweimal wöchentlich vor und nach Inokulation gesammelt. Niveaus der Leberenzyme Serumalanin-Aminotransferase (ALT), Isocitratdehydrogenase (ICD) und Gamma-Glutamyltransferase (GGT) wurden mit kommerziell erhältlichen Tests (Medpath Inc., Rockville, MD) bestimmt. Serologische Tests wurden wie vorstehend beschrieben durchgeführt.
- BEISPIEL 1
- Identifizierung der DNA-Sequenz des Genoms des HEV-Stamms SAR-55.
- Herstellung einer Virus-RNA-Matrize für PCR. Galle von einem HEV-infizierten Cynomolgus-Affen (10 µl), 20% (Gewicht/Volumen) SDS (auf eine Endkonzentration von 1%), Proteinase K (10 mg/ml; auf eine Endkonzentration von 1 mg/ml), 1 µl tRNA (10 mg/ml) und 3 µl 0,5 M EDTA wurden in einem Endvolumen von 250 µl gemischt und 30 Minuten bei 55°C inkubiert. Gesamt-Nukleinsäuren wurden von der Galle zweimal mit Phenol/Chloroform, 1:1 (Volumen/Volumen) bei 65°C und einmal mit Chloroform extrahiert, dann durch Ethanol präzipitiert, mit 95% Ethanol gewaschen und für eine RT-PCR verwendet. RT-PCR-Amplifikation von HEV-RNA aus Fäkalien und insbesondere aus Seren war wirksamer, wenn die RNA umfangreicher gereinigt wurde. Serum (100 µl) oder eine 10%ige fäkale Suspension (200 µl) wurde wie vorstehend mit Proteinase K behandelt. Nach einer 30-minütigen Inkubation wurden 300 µl eines CHAOS-Puffers (4,2 M Guanidinthiocyanat/0,5 N-Lauroylsarcosin/0,025 M Tris-HCl, pH 8,0) zugegeben. Nukleinsäuren wurden zweimal mit Phenol/Chloroform bei 65°C gefolgt von einer Chloroformextraktion bei Raumtemperatur extrahiert. Dann wurde 7,5 M Ammoniumacetat (225 µl) zu der oberen Phase gegeben und Nukleinsäuren wurden mit 0,68 ml 2-Propanol präzipitiert. Der Niederschlag wurde in 300 µl CHAOS-Puffer gelöst und 100 µl H2O wurden zugegeben. Chloroformextraktion und 2-Propanolpräzipitation wurden wiederholt. Nukleinsäuren wurden in Wasser gelöst, mit Ethanol präzipitiert, mit 95% Ethanol gewaschen und für eine RT-PCR verwendet.
- Primer. Vierundneunzig Primer, 21–40 Nukleotide (nt) lang und komplementär zu den Plus- oder Minus-Strängen des Genoms eines HEV-Stamms aus Burma (BUR-121) (Tam, A. W. et al. (1991), Virology, 185: 120–131) oder des SAR-55-Genoms, wurden unter Verwendung eines DNA-Synthetisierers Modell 391 von Applied Biosystems synthetisiert.
- Die Sequenzen dieser 94 Primer sind startend mit SEQ ID NO: 5 und fortsetzend bis SEQ ID NO: 98 nachstehend gezeigt:
- Die Abkürzungen links von den Sequenzen stellen das folgende dar: R und D bezeichnen reverse bzw. Vorwärts-Primer; B und S bezeichnen Sequenzen, die von dem Burma-121-Stamm von Hepatitis E bzw. dem SAR-55-Stamm von Hepatitis E abgeleitet sind; 5'NC und 3'NC bezeichnen 5'- bzw. 3'-nicht-kodierende Regionen des HEV-Genoms; und 1, 2 und 3 bezeichnen Sequenzen, die von den offenen Leserahmen 1, 2 bzw. 3 abgleitet sind. Das Symbol () rechts von manchen Sequenzen zeigt eine Insertion einer künstlichen Restriktionsschnittstelle in diesen Sequenzen an.
- Zum Klonieren von PCR-Fragmenten wurden EcoRI-, BamHI- oder BglII-Restriktionsschnittstellen, die von 3–7 nt angeführt wurden, an das 5'-Ende von Primern angefügt.
- RT-PCR. Das gewöhnliche 100-µl RT-PCR-Gemisch enthielt eine Matrize, 10 mM Tris-HCl (pH 8,4), 50 mM KCl, 2,5 mM MgCl2, alle vier dNTPs (jeweils mit 0,2 mM), 50 pmol direkter Primer, 50 pmol reverser Primer, 40 Einheiten RNasin (Promega), 16 Einheiten reverse Transkriptase aus Vogel-Myeloblastose-Virus (Promega), 4 Einheiten AmpliTaq (Cetus), unter 100 µl Leicht-Mineralöl. Das Gemisch wurde eine Stunde bei 42°C inkubiert, und dann durch 35 PCR-Zyklen, eine Minute bei 94°C, eine Minute bei 45°C und eine Minute bei 72°C, amplifiziert. Die PCR-Produkte wurden auf 1%igen Agarose-Gelen analysiert.
- Klonieren von PCR-Fragmenten. PCR-Fragmente, die Restriktionsschnittstellen an den Enden enthielten, wurden mit den Restriktionsenzymen EcoRI und BamHI oder EcoRI und BglII verdaut und in EcoRI/BamHI-verdautem pBR322 oder pGEM-3Z (Promega) kloniert. Alternativ wurden PCR-Fragmente in pCR1000 (Invitrogen) unter Verwendung des TA-Klonierkits (Invitrogen) kloniert.
- Sequenzieren von PCR-Fragmenten und Plasmiden. PCR-Fragmente wurden aus 1%igen Agarose-Gelen ausgeschnitten und durch Geneclean (Bio 101, La Jolla, CA) gereinigt. Doppelsträngige PCR-Fragmente wurden unter Verwendung von Sequenase (United States Biochemical) wie in Winship, P. R. (1984), Nucleic Acids Rev., 17: 1266 beschrieben sequenziert. Doppelsträngige Plasmide, die durch CsCl-Gradienten gereinigt wurden, wurden mit einem Sequenase-Kit (United States Biochemical) sequenziert.
- Computeranalyse von Sequenzen. Nukleotidsequenzen von HEV-Stämmen wurden unter Verwendung des Software-Pakets der Genetics Computer Group (Madison, WI) verglichen (Devereaux, J. et al. (1984), Nucleic Acids Rev., 12: 387–395, Version 7.5, auf einem VAX 8650-Computer (am National Cancer Institute, Frederick, MD)).
- BEISPIEL 2
- Konstruktion eines rekombinanten Expressionsvektors, P63-2.
- Ein Plasmid, das den gesamten ORF-2 des Genoms des HEV-Stamms SAR-55 (Tsarev, S. A. et al. (1992), Proc. Natl. Acad. Sci. USA, 89: 559–563) enthielt, wurde verwendet, um ein Nrul-BglII-Restriktionsfragment zu erhalten. NruI schnitt die HEV-cDNA fünf Nukleotide stromaufwärts des ATG-Initiationscodons des ORF-2. Eine künstliche BglII-Stelle war vorher am 3'-Ende des HEV-Genoms direkt vor der Poly-A-Sequenz platziert worden (Tsarev, S. A. et al. (1992), Proc. Natl. Acad. Sci. USA, 89: 559–563). Zum Inserieren dieses Fragments in einen pBlueBac-Transfervektor (Invitrogen) wurde ein synthetischer Polylinker in die einzelne NheI-Stelle in dem Vektor eingefügt. Dieser Polylinker enthielt BlnI- und BglII-Stellen, die sowohl in den HEV-cDNA- als auch den pBlueBac-Sequenzen nicht vorkommen. Das NruI-BglII-ORF-2-Fragment wurde in BlnI-BglII-pBlueBac unter Verwendung eines Adapters wie in
1 gezeigt inseriert. - BEISPIEL 3
- Expression von P63-2 in SF9-Insektenzellen.
- p63-2 und AcMNPV-Baculovirus-DNA (Invitrogen) wurden in SF9-Zellen (Invitrogen) durch das Ca-Präzipitationsverfahren gemäß dem Invitrogen-Protokoll co-transfiziert – durch Folgen dieses Protokolls kann die AcMNPV-Baculovirus-DNA einen lebenden intakten Baculovirus produzieren, der p63-2 zur Bildung eines rekombinanten Baculovirus verpacken kann. Dieser rekombinante Baculovirus wurde viermal Plaque-gereinigt. Der erhaltene rekombinante Baculovirus 63-2-IV-2 wurde zur Infektion von SF9-Zellen verwendet.
- SDS-PAGE und Western Blot. Insektenzellen wurden in Beladungspuffer (50 mM Tris-HCl, pH 6,8, 100 mM DTT, 2% SDS, 0,1% Bromphenolblau und 10% Glycerin) resuspendiert und eine SDS-Polyacrylamidgelelektrophorese wurde wie in Laemmli, U. K. (1970), Nature, 227: 680 beschrieben durchgeführt. Gele wurden mit Coomassie-Blau angefärbt oder Proteine wurden auf BA-85-Nitrocellulosefilter (Schleicher & Schuell) elektrogeblottet. Nach Transfer wurden Nitrocellulosemembranen in PBS geblockt, das 10% fötales Kälberserum und 0,5% Gelatine enthielt. Als ein Primärantikörper wurde 1:1000 verdünntes Hyperimmunserum von Schimpanse-1313 verwendet. Als ein Sekundärantikörper wurde 1:2000 verdünnter Phosphatasemarkierter Affinitäts-gereinigter Ziegenantikörper gegen humanes IgG (Kirkegaard & Perry Laboratories, Inc.) verwendet. Filter wurden in mit Western-Blue stabilisiertem Substrat für alkalische Phosphatase (Promega) entwickelt. Alle Inkubationen wurden in Blockierlösung und Waschschritte mit PBS mit 0,05% Tween-20 (Sigma) durchgeführt.
- Expression von HEV-ORF-2. Das Hauptprotein, das in mit rekombinanten Baculovirus 63-2-IV-2 infizierten SF9-Zellen synthetisiert wurde, war ein Protein mit einem scheinbaren Molekulargewicht von 74 kD (
2A , Spur 3). Diese Größe ist ein bisschen größer als die für das gesamte ORF-2 vorhergesagte (71 kD). Der Größenunterschied könnte durch Glykosylierung des Proteins begründet sein, da mindestens eine potentielle Glykosylierungsstelle (Asn-Leu-Ser) im N-terminalen Teil vorhanden ist. Dieses Protein wurde nicht in nicht-infizierten Zellen (2A , Spur 1) oder in Zellen, die mit Wildtyp nicht-rekombinantem Baculovirus infiziert waren (2A , Spur 2), nachgewiesen. In letzterem Fall war das nachgewiesene Hauptprotein ein Polyhedron-Protein. Wenn dieselben Lysate durch Western Blot (2B ) mit Serum von Chimp-1313 (hyperimmunisiert mit HEV) analysiert wurden, reagierten nur Proteine in dem rekombinanten Zell-Lysat (Spur 3) und die Hauptbande wurde wieder durch ein 74 kD-Protein dargestellt (2B ). Nebenbanden von etwa 25, 29, 35, 40–45 und 55–70 kDa, die in dem Coomassie-gefärbten Gel vorhanden waren (2A , Spur 3), reagierten auch mit Serum im Western Blot (2B , Spur 3). Manche der Banden mit Molekulargewichten, die größer als 74 kDa waren, waren auf unterschiedliche Ausmaße der Glykosylierung zurückzuführen, während die Banden mit geringerem Molekulargewicht Prozessierung und/oder Abbau widerspiegeln könnten. Serum, das von Chimp-1313 vor Inokulation mit HEV erhalten wurde, reagierte im Western Blot mit keinem der Proteine. - BEISPIEL 4
- Immun-Elektronenmikroskopie von rekombinanten infizierten SF9-Zellen.
- 5 × 106 rekombinante infizierte SF9-Zellen wurden in CsCl (1,30 g/ml) mit 10 mM Tris-HCl, pH 7,4, 0,3% Sarcosyl mit Ultraschall behandelt und 68 h bei 40000 UpM (SW60Ti) zentrifugiert. 50 µl der Fraktion, die die höchste ELISA-Antwort und eine Schwimmdichte von 1,30 g/ml aufwies, wurde in 1 ml PBS verdünnt und 5 µl Hyperimmunserum aus Chimp-1313 wurde zugegeben. Das Hyperimmunserum wurde durch Wiederbelastung eines vorher infizierten Schimpansen mit einem zweiten Hepatitis E-Stamm (mexikanischer HEV) hergestellt. Proben wurden eine Stunde bei Raumtemperatur und dann über Nacht bei 4°C inkubiert. Immunkomplexe wurden unter Verwendung eines SW60Ti-Rotors bei 30000 UpM und 4°C zwei Stunden präzipitiert. Niederschläge wurden in destilliertem Wasser resuspendiert, mit 3% PTA negativ angefärbt, auf Kohlenstoffgitter platziert und bei einer Vergrößerung von 40000 in einem Elektronenmikroskop, EM-10, Carl Zeiss, Oberkochen, Deutschland, untersucht.
- Nachweis von VLPs. Zell-Lysate von Insektenzellen, die mit Wildtyp oder rekombinantem Baculovirus 63-2-IV-2 infiziert worden waren, wurden durch CsCl-Dichte zentrifugation fraktioniert. Wenn Fraktionen des CsCl-Gradienten von den rekombinanten infizierten Insektenzellen mit Hyperimmunserum von Chimp-1313 inkubiert wurden, wurden zwei Arten an Virus-Like-Partikeln (VLP), die mit Antikörpern bedeckt waren, in der Fraktion mit einer Schwimmdichte von 1,30 g/ml beobachtet: zum ersten (
3A ) Antikörper-bedeckte einzelne Partikel, die eine Größe (30 nm) und morphologische Struktur hatten, die auf HEV hindeuteten, zum zweiten (3B ) Antikörper-beschichtete Aggregate von Partikeln, die kleiner als HEV waren (etwa 20 nm), aber die ansonsten HEV ähnelten. Direkte EM zeigte die Anwesenheit einer sehr heterogenen Population an Objekten, die manche mit einem Durchmesser von 30 bzw. 20 nm umfasste, die wie Viruspartikel aussahen, aber in Abwesenheit von gebundenem Antikörper nicht als HEV bestätigt werden konnten. Eine Anzahl an IEM-Experimenten legte nahe, dass mindestens manche der Proteine, die von der ORF-2-Region des HEV-Genoms synthetisiert wurden, sich zu einer Partikelstruktur zusammengesetzt hatten. Es wurde beobachtet, dass Insektenzellen zu einer späteren Phase der Infektion, wenn das Verhältnis von kleineren Proteinen größer war, durchgehend bessere Ergebnisse im ELISA ergaben. Daher wurden nicht fraktionierte Lysate von rekombinanten Insektenzellen von einer späteren Phase der Infektion als Antigen in ELISA in nachfolgenden Tests verwendet. - BEISPIEL 5
- Nachweis durch ELISA, basierend auf Antigen von Insektenzellen, die komplettes ORF-2 exprimieren, von Anti-HEV nach Infektion mit unterschiedlichen Stämmen von HEV.
- 5 × 106 SF9-Zellen, die mit 63-2-IV-2-Virus infiziert worden waren, wurden in 1 ml 10 mM Tris-HCl, pH 7,5, 0,15 M NaCl resuspendiert und dann dreimal eingefroren und aufgetaut. 10 µl dieser Suspension wurden in 10 ml Carbonatpuffer (pH 9,6) gelöst und zum Bedecken einer flexiblen Mikroliter-Assayplatte (Falcon) verwendet. Serumproben wurden 1:20, 1:400 und 1:8000 oder 1:100, 1:1000 und 1:10000 verdünnt. Die gleichen Blockier- und Waschlösungen wie für den Western Blot beschrieben wurden im ELISA verwendet. Als ein Sekundärantikörper wurde eine Peroxidase-konjugierte Ziege-IgG-Fraktion gegen humanes IgG oder ein Meerrettichperoxidase-markiertes Ziege-Anti-Alt- oder Anti-Neuweltaffe-Immunoglobulin verwendet. Die Ergebnisse wurden durch Messung der optischen Dichte (O. D.) bei 405 nm bestimmt.
- Zur Bestimmung, ob Insektenzell-abgeleitetes Antigen, das einen Pakistani-Stamm von HEV darstellt, einen Anti-HEV-Antikörper in Cynomolgus-Affen, die mit dem mexikanischen Stamm von HEV infiziert waren, nachweisen konnte, wurden drei Affen untersucht (
4 ). Zwei Affen, Cyno-80A82 und Cyno-9A97, wurden mit Fäkalien infiziert, die den Mexiko '86-HEV-Stamm (Ticehurst, J. et al. (1992), J. Infect. Dis., 165: 835–845) enthielten, und der dritte Affe, Cyno-83, wurde mit einer zweiten Passage des gleichen Stamms infiziert. Als eine Kontrolle wurden Serumproben von Cyno-374, der mit dem Pakistani-HEV-Stamm SAR-55 infiziert war, in dem gleichen Experiment getestet. Alle drei Affen, die mit dem mexikanischen Stamm infiziert wurden, serokonvertierten zu Anti-HEV. Tiere der ersten Passage serokonvertierten bis Woche 15 und der zweiten Passage bis Woche 5. Interessanterweise wurde der höchste Anti-HEV-Titer unter den vier Tieren in Cyno-83 gefunden, der mit der zweiten Passage des mexikanischen Stamms inokuliert war. Cynos, die mit der ersten Passage des mexikanischen Stamms inokuliert waren, entwickelten die niedrigsten Titer, während diejenigen, die mit der ersten Passage des Pakistani-Stamms inokuliert waren, mittlere Titer entwickelten. - BEISPIEL 6
- Spezifität von Anti-HEV-ELISA, basierend auf Antigen von Insektenzellen, die komplettes ORF-2 exprimieren.
- Um abzuschätzen, ob der hier beschriebene ELISA spezifisch Anti-HEV unter Ausschluss eines jeglichen anderen Typs von Hepatitis-verwandten Antikörpern nachweist, wurden Serumproben aus Schimpansen in Sätzen aus vier analysiert, die mit den anderen bekannten Hepatitisviren infiziert waren (Garci, P. et al. (1992) J. Infect. Dis., 165: 1006–1011; Farci, P. et al. (1992), Science (im Druck); Ponzetto, A. et al. (1987) J. Infect. Dis., 155: 72–77; Rizzetto, M. et al. (1981) Hepatology 1: 567–574; Referenz für Chimps–1413, 1373, 1442, 1551 (HAV); und für Chimps-982, 1442, 1420, 1410 (HBV) sind nicht publizierte Daten von Purcell et al.) (Tabelle 1). Proben von Seren vor Inokulation und 5 Wochen und 15 Wochen nach Inokulation wurden in einem HEV-ELISA bei Serumverdünnungen von 1:100, 1:1000 und 1:10000 analysiert. Keines der Seren von Tieren, die mit HAV, HBV, HCV und HDV infiziert waren, reagierte in ELISA auf HEV-Antikörper, aber alle 4 Schimpansen, die mit HEV inokuliert waren, entwickelten die IgM- und IgG-Klassen für Anti-HEV.
- BEISPIEL 7
- Bestimmung des Wirtsbereichs des SAR-55-Stamms von HEV in nicht-menschlichen Primaten.
- Unterschiedliche Primatenspezies wurden intravenös mit einer Standard-Stuhlsuspension von HEV inokuliert und fortlaufende Serumproben wurden zur Kontrolle auf eine Infektion gesammelt. Serum-ALT-Niveaus wurden als ein Indikator für Hepatitis bestimmt, während Serokonvertierung als ein Anstieg von Anti-HEV definiert wurde. Die Ergebnisse wurden mit denjenigen verglichen, die in Cynomolgus-Affen und Schimpansen erhalten wurden.
- Beide Rhesusaffen, die mit HEV inokuliert wurden (Tabelle 2), zeigten sehr deutliche Peaks an Alanin-Aminotransferase-Aktivität sowie eine starke Anti-HEV-Antwort. Der Peak an Alanin-Aminotransferase-Aktivität wurde an Tag 35 für beide Tiere beobachtet und eine Serokonvertierung trat an Tag 21 auf. Der maximale Titer an Anti-HEV wurde an Tag 29 erreicht. Beide grünen Meerkatzen, die in dieser Studie verwendet wurden (Tabelle 2), entwickelten erhöhte Alanin-Aminotransferase-Aktivität und Anti-HEV. Obwohl grüne Meerkatze 230 sieben Wochen nach Inokulation starb, wurde ein Beweis einer Infektion vor diesem Zeitpunkt erhalten. Peak-Alanin-Aminotransferase-Aktivität für Affe 74 übertraf den Durchschnittswert von Seren vor Inokulation etwa dreifach und für Affe 230 etwa fünffach. Peaks an Alanin-Aminotransferase-Aktivität und Serokonvertierung erschienen gleichzeitig an den Tagen 28 und 21 in Affen 74 bzw. 230. Tabelle 2. Biochemische und serologische Profile von HEV-Infektion in acht Primatenspezies.
Alanin-Aminotransferase (Einheiten/l) Anti-HEV-IgG Tier Vor Inokulation, Durchschnitt (SD) Tag Wert Tag des ersten Nachweises (Titer) Maximaler Titer Schimpanse 1374 51(12) 27 114 27(1:400) 1:8000 1375 41(14) 27 89 27(1:400) 1:8000 Cynomolgus-Affe 374* 46(20) 26 608 19(1:400) 1:8000 381* 94(19) 35 180 28(1:20) 1:8000 Rhesusaffe 726 43(6) 35 428 21(1:20) 1:8000 938 29(10) 35 189 21(1:20) 1:8000 Grüne Meerkatze 74 72(21) 28 141 28(1:400) 1:8000 230 102(45) 21 334 21(1:8000) 1:8000 Schweinsaffe 98 37(8) 21 47 21(1:400) 1:8000 99 41(6) 28 59 21(1:400) 1:8000 Tamarin 616 28(7) 70 41 - 636 19(4) 7, 56 30 - Totenkopfaffe 868 90(35) 40 355 41(1:20) 1:20 869 127(63) 42 679 35(1:20) 1:20 Nachtaffe 924 41(7) 35 97 21(1:20) 1:8000 925 59(6) 49,91† 78,199 † 21(1:20) 1:8000 - BEMERKUNG. – kein Anti-HEV nachgewiesen.
- * Vorher untersucht unter Verwendung von Fragmenten von HEV-Proteinen, die in Bakterien exprimiert wurden, als Antigen [18].
- † Biomodale Erhöhung der Alanin-Aminotransferase.
- SD = Standardabweichung.
- Schweinsaffe 99 zeigte eine Erhöhung der Alanin-Aminotransferase-Aktivität > 3 SD über dem Mittelwert von Seren vor Inokulation, während Schweinsaffe 98 dies nicht zeigte. Jedoch serokonvertierten beide Affen an Tag 21 und die Anti-HEV-Titer waren äquivalent zu denjenigen der Schimpansen und Altweltaffen. Aufgrund der geringen Peak-Alanin-Aminotransferase-Werte in den Schweinsaffen kann die Möglichkeit einer Immunisierung anstatt einer Infektion mit HEV nicht komplett ausgeschlossen werden. Jedoch ist eine Immunisierung wegen mehrerer Gründe unwahrscheinlich. Zum einen wurde keine Immunisierung in den zwei Tamarinen, die nur ein Viertel so groß wie die Schweinsaffen sind, aber die gleiche Menge an Inokulum erhielten, beobachtet. Zum zweiten ist es bekannt, dass die Menge an HEV, die in Fäkalien ausgeschieden wird, normalerweise sehr gering ist, und 0,5 ml der 10%igen Fäkaliensuspension, die in dieser Studie verwendet wurde, enthält wahrscheinlich keine Menge an Antigen, die ausreichend ist, ein Tier zu immunisieren, insbesondere wenn es intravenös inokuliert wird.
- Kein in dieser Studie inokulierter Tamarin zeigte einen signifikanten Anstieg an Alanin-Aminotransferase-Aktivität oder eine Entwicklung von Anti-HEV (Tabelle 2). Daher waren diese Tiere anscheinend nicht infiziert. Die Totenkopfaffen entwickelten Anti-HEV, allerdings mit einem signifikant geringeren Niveau als Schimpansen oder Altweltaffen (Tabelle 2). Zusätzlich erfolgte Serokonvertierung in anderen Tieren später. Totenkopfaffe 868 serokonvertierte an Tag 41 und 869 an Tag 35. Der Anti-HEV-Titer war nicht > 1:20 zu einem jeglichen Zeitpunkt während > 3 Monaten Beobachtung und war deutlich abnehmend in beiden Tieren, nachdem er einen Peakwert an Tagen 47–54 erreicht hatte. Jedoch waren die Anstiege von Alanin-Aminotransferase-Aktivität in beiden Tieren ziemlich deutlich und standen zeitlich in Bezug zu der Zeit der Serokonvertierung.
- Die Nachtaffen antworteten auf HEV-Infektion etwa so gut wie die Altweltaffen-Spezien (Tabelle 2). Beide Nachtaffen serokonvertierten an Tag 21 und bis Tag 28 hatte der Anti-HEV-Titer einen Wert von 1:8000 erreicht. Alanin-Aminotransferase-Aktivität erreichte einen Peak an Tag 35 bei Nachtaffe 924 aber nicht vor Tag 49 bei Affe 925.
- BEISPIEL 8
- Nachweis von IgM- und IgG Anti-HEV in Schimpansen.
- In beiden Schimpansen erhöhten sich die Serum-ALT-Niveaus etwa vier Wochen nach Inokulation (Tabelle 2,
5 ). Beide Schimpansen serokonvertierten zum Zeitpunkt der ALT-Enzymerhöhung oder früher (5A ,5C ). Niveaus an IgM-Anti-HEV wurden für die Schimpansen auch bestimmt. Bei Chimp-1374 war der Titer an IgM-Anti-HEV (5B ) nicht so hoch wie der IgG-Titer (5A ) und nahm über zwei Wochen ab. Obwohl sowohl IgG- als auch IgM-Antikörper für dieses Tier zuerst an Tag 20 nachgewiesen wurden, war der Titer an IgM-Anti-HEV an diesem Tag am höchsten, während der Titer an IgG am geringsten war, dann aber anstieg und bei ungefähr demselben Niveau für mehr als drei Monate blieb. Bei Chimp-1375 wurde nur IgM-Anti-HEV an Tag 20 nachgewiesen (5D ). Der Titer war höher als bei Chimp-1374 und IgM-Anti-HEV wurde während des gesamten Beobachtungszeitraums nachgewiesen. IgG-Anti-HEV wurde in diesem Tier erstmals an Tag 27 beobachtet (5C ) und blieb während des Experiments bei etwa dem gleichen Niveau. - BEISPIEL 9
- Vergleich von ELISA, der auf in Insektenzellen exprimiertem komplettem ORF-2-Protein basiert, mit dem, der auf in E. coli exprimierten Fragmenten von strukturellen Proteinen basiert.
- Um abzuschätzen, ob eine Expression der gesamten ORF-2-Region des HEV-Genoms in eukaryotischen Zellen einen Vorteil gegenüber Expression von Fragmenten von strukturellen Proteinen in E. coli aufweist, verwendeten wir das erstgenannte Antigen in einem ELISA, um Cynomolgus-Affen-Seren, die vorher unter Verwendung der in Bakterien exprimierten Antigenfragmente analysiert worden waren (Tsarev, S. A. et al. (1992) Proc. Natl. Acad. Sci. USA, 89: 559–563 und Tsarev, S. A. et al. (1993) J. Infect. Dis. (167: 1302–1306)), erneut zu testen (Tabelle 3). Tabelle 3. Vergleich von ELISA, der auf Antigen aus Insektenzellen basiert, die kompletten ORF-2 exprimieren, mit dem, der auf Antigen aus E. coli basiert, das Fragmente von strukturellen Proteinen exprimiert
Cyno # Von Bakterienzellen abgeleitetes Antigen (Teil von OFR-2)* Von Insektenzellen abgeleitetes Antigen (kompletter ORF-2) Anti-HEV Tag des ersten Anti-HEVNachweises Tag des ersten Nachweises Titer Max. Titer Cyno-376 28 21 1:400 1:8000 Cyno-369 54 40 1:100 1:8000 Cyno-374 19 19 1:400 1:8000 Cyno-375 26 26 1:400 1:8000 Cyno-379 21 19 1:100 1:8000 Cyno-381 28 28 1:400 1:8000 - * Die Seren wurden auch mit weniger sensitivem ORF-3-Antigen getestet.
- Tsarev, S. A. et al. (1993), J. Infect. Dis. 168: 369–378
- Bei drei der sechs durch ELISA untersuchten Affen wies das in Insektenzellen exprimierte Antigen eine Serokonvertierung früher als das in E. coli exprimierte Antigen nach. Unter Verwendung des Insektenzell-abgeleiteten Antigens waren wir fähig, Anti-HEV-Antikörper in Seren von allen sechs Affen bei der höchsten getesteten Verdünnung (1:8000) nachzuweisen. Mit E. coli-Zell-abgeleitetem Antigen (Burma-Stamm) wurde keine Information über Anti-HEV-Titer erhalten, da alle Seren nur bei einer Verdünnung von 1:100 getestet wurden (Tsarev, S. A. et al. (1992) Proc. Nat. Acad. Sci. USA, 89: 559–563; Tsarev et al. (1993) J. Infect. Dis. (167: 1302–1306)).
- In einer anderen Studie wurde Hepatitis E-Virus, Stamm SAR-55, in zehnfachen Schritten seriell verdünnt und die 10–1- bis 10–5-Verdünnungen wurden in Paare von Cynomolgus-Affen inokuliert, um Virustiter zu erzeugen. Die Serum-ALT-Niveaus wurden zur Bestimmung von Hepatitis gemessen und ein Serum-Antikörper gegen HEV wurde durch das ELISA-Verfahren (Daten in den Abbildungen) oder durch einen ELISA von Genelab (drei ELISAs, wobei jeder auf einem der Antigene basiert, die in Yarbrough et al. (J. Virol., (1991) 65: 5790–5797) als 4-2, 3-2 und 612 bezeichnet sind) (Daten sind als positiver (+) oder negativer (–) Test am unteren Rand der
6a –g gezeigt) bestimmt. Alle Proben wurden kodiert getestet. - Das ELISA-Verfahren wies Serokonvertierung zu IgG-Anti-HEV in allen inokulierten Cynos und bei allen Verdünnungen des Virus nach.
- Im Gegensatz dazu waren die Ergebnisse von Genelab auffallend variabel wie nachstehend zusammengefasst. Tabelle 4.
Verdünnung des Virus ELISA von Genelab ELISA 10–1 kein Testergebnis positiv 10–2 positiv für beide Tiere, eingeschränkte Dauer positiv 10–3 negativ für beide Tiere positiv 10–4 Cyno 389: positiv für IgM und IgG positiv Cyno 383: negativ positiv 10–5 Cyno 386: negativ positiv Cyno 385: positiv positiv - Da Cyno 385 (10–5) in ELISA-Tests sowohl durch Genelabs als auch wie hierin beschrieben positive war, würden auch 10–4 (zehnfach mehr Virus inokuliert) und 10–3 (100-fach mehr Virus inokuliert) als positiv zu erwarten sein. Der wie hierin beschriebene ELISA wertete sie im Gegensatz zu dem ELISA-Test von Genelab als positiv, der beide positiven bei 10–3 und einen bei 10–4 nicht erkannte, obwohl die ALT-Niveaus von Cyno 383 und 393 eine aktive Hepatitis nahe legten. Daher unterstützen die Daten die Vorteile des vorliegenden ELISA-Verfahrens gegenüber den Verfahren zum Nachweis von Antikörpern gegen HEV des Stands der Technik.
- BEISPIEL 10
- Vergleich von ELISAs, die auf rekombinanten ORF-2-Antigenen basieren, die entweder aus einem 55 kDa-Protein, das von der gesamten ORF-2-Region des Pakistani-HEV-Stamms SAR-55 exprimiert wird, oder aus kürzeren Regionen von ORF-2, die als Fusionsproteine in Bakterien exprimiert werden, bestehen.
- Wie in Beispiel 3 beschrieben und in
2A und2B gezeigt, wird eine Anzahl an Proteinen mit variierenden Molekulargewichten in Insektenzellen exprimiert, die mit dem rekombinanten Baculovirus, das den gesamten ORF-2 enthält, infiziert sind. Ein Protein mit einem Molekulargewicht von ungefähr 55 kDa wurde von 5 × 108 SF-9-Zellen, die sieben Tage nach Inokulation geerntet wurden, wie folgt teilweise gereinigt: die infizierten Zellen wurden zentrifugiert, in 10 ml 10 mM Tris-HCl (pH 8,0), 50 mM NaCl mit 40 µg/ml Phenylmethylsulfonylfluorid (Sigma, St. Louis, Missouri) resuspendiert, zum Aufbrechen der Zellen mit Ultraschall behandelt, und das Lysat wurde bei 90 000 × g bei 4°C 30 Minuten zentrifugiert. Der Überstand wurde auf eine DEAE-Sepharose CL-6B (Pharmacia, Uppsala, Schweden)-Säulen gegeben, die mit 10 mM Tris-HCl (pH 8,0), 50 mM NaCl äquilibriert war. Die Säule wurde mit Beladungspuffer gewaschen und das 55 kDa-Protein wurde in 10 mM Tris-HCl (pH 8,0), 250 mM NaCl eluiert. Fraktionen, die das 55 kDa-Protein enthielten, wurden vereinigt, und das Protein wurde durch Zugabe von 3 g (NH4)2SO4 zu 10 ml der Proteinlösung ausgefällt. Der Proteinniederschlag wurde in 10 mM Tris-HCl (pH 8,0), 50 mM NaCl gelöst. Das 55 kDa-Protein wurde dann als das Insektenzell-exprimierte HEV-Antigen im ELISA in einem Vergleichstest gegen ELISAs, die auf einem der zwei HEV-Antigene basierten, die in Bakterien exprimiert wurden (3-2 (Mexiko) (Goldsmith et al., (1992) Lancet, 339: 328–331) oder SG3 (Burma) (Yarbough et al., (1993) Assay Development of diagnostics tests for hepatitis E. In "International Symposium an Viral Hepatitis and Liver Disease. Scientific program and abstract volume." Tokyo:VHFL, S. 87, Abstract # 687), verwendet. Diese bakteriellen Antigene waren Fusionsproteine aus der 26 kDa-Glutathion-S-Transferase (GST) und entweder der antigenen Sequenz 3-2 (M), die aus 42 Aminosäuren besteht, die 6 Aminosäuren stromaufwärts des C-Terminus von ORF-2 liegen (Yarbough et al., (1991) J. Virol., 65: 5790–5797), oder den 327 C-terminalen Aminosäuren von ORF-2 (Yarbough et al., (1993)). Die ELISAs wurden wie folgt durchgeführt. - 60 ng pro Näpfchen des 55 kDa-Proteins oder 200 ng pro Näpfchen der Fusionsantigene in Carbonatpuffer (pH 9,6) wurden in Näpfchen einer Polystyrol-Mikrotiter-Assayplatte (Dynateck, S. Windham, ME) zwei Stunden bei 37°C inkubiert. Platten wurden mit PBS mit 10% fötalem Kälberserum und 0,5% Gelatine blockiert. Serumproben von Cynomolgus-Affen, die intravenös (beachte: Cynos 387 und 392 wurden oral inokuliert) mit einer Verdünnung von Fäkalien, die den HEV-Stamm SAR-55 enthielten, von 10–1 bis 10–8 wie in Tabelle 5 und
7A –7J und8A –8D angegeben inokuliert wurden, wurden 1:100 in Blockierlösung verdünnt. 1:1000 oder 1:2000 verdünnter Peroxidase-konjugierter Ziege-Anti-Mensch-IgM (Zymed, San Francisco, CA) oder 1:1000 verdünntes Peroxidase-markiertes Ziege-Anti-Mensch-Immunoglobulin wurde als der Nachweis-Antikörper verwendet. - In all diesen ELISA-Tests, außer demjenigen für die oral inokulierten Affen, Cyno-387 und Cyno-392, wurden die 55 kDa- und die Fusions-Antigene gleichzeitig im selben Labor getestet, so dass die einzige Variable das verwendete Antigen war. Kriterien zum Bewerten positiver Reaktionen in Anti-HEV-ELISA mit dem 55 kDa-Antigen waren ein optischer Dichtewert ≥ 0,2 und mehr als doppelt so groß wie der einer Vor-Inokulations-Serumprobe desselben Tiers. Da beide Antigene, die in Bakterien exprimiert wurden, Fusionsproteine mit GST waren, musste die optische Dichte einer Probe, die mit diesen Antigenen getestet wurde, zusätzlich dreifach höher als die sein, die mit nicht-fusioniertem GST erhalten wurde, um als positiv angesehen zu werden (Goldsmith et al., (1992)).
- ERGEBNISSE
- Beide Cynomolgus-Affen (377, 378), die mit der 10–1-Verdünnung der fäkalen Standard-Suspension von HEV inokuliert worden waren, zeigten eine ausgeprägte Erhöhung der ALT-Aktivität 4–5 Wochen nach Inokulation, was Hepatitis anzeigt (Tabelle 5,
7A und7B ). - Alle drei getesteten Antigene wiesen IgM-Anti-HEV in Proben, die von Cyno-377 genommen wurden, drei Wochen nach Inokulation nach (Tabelle 5,
8A ), aber IgM-Anti-HEV wurde nicht in Proben des zweiten Tiers, Cyno-378, nachgewiesen. IgG-Anti-HEV wurde in beiden Tieren mit dem 55 kDa-basierten ELISA aber nur in Cyno-377 mit dem ELISA, der auf Fusionsantigenen basierte, nachgewiesen. OD-Werte für IgG-Anti-HEV waren deutlich höher als diejenigen für IgM-Anti-HEV. ELISA-Werte, die mit dem 55 kDa-Antigen erhalten wurden, waren auch deutlich höher als diejenigen, die mit einem der beiden Fusionsantigene erhalten wurden (7A und7B ). Die Muster der OD-Werte, die im ELISA mit Antigenen von den beiden Quellen beobachtet wurden, unterschieden sich auch deutlich. Im Falle des auf den Fusionsantigenen basierten ELISA erreichten positive Signale kurz nach Serokonvertierung ein Maximum und verringerten sich dann während der 15 Wochen des Experiments. Bei dem auf dem 55 kDa-Antigen basierten ELISA erreichte das positive Signal kurz nach Serokonvertierung ein Maximum und blieb während des Experiments (15 Wochen) bei ungefähr dem gleichen hohen Niveau. - Erhöhung der ALT-Aktivitäten in beiden Affen (394 und 395), die mit einer 10–2-Verdünnung der Standard-HEV-Stuhlsuspension inokuliert worden waren, war zum erwarteten Zeitpunkt der Hepatitis deutlich weniger ausgeprägt als in Tieren, die mit der zehnfach höheren Dosis inokuliert worden waren (Tabelle 5,
7C und7D ). Cyno-395 hatte sogar sowohl vor Inokulation als auch 15 Wochen nach Inokulation höhere ALT-Aktivitäten. Die letztgenannte war wahrscheinlich nicht durch eine HEV-Infektion bedingt. Wöchentliches positives IgM-Anti-HEV wurde nur in Cyno-394 (8B ) und nur mit dem auf dem 55 kDa-Antigen basierten ELISA nachgewiesen. Jedoch waren beide Tiere infiziert, da IgG-Anti-HEV-Serokonvertierung in beiden Tieren nachgewiesen wurde. In Cyno-394 wurde Anti-HEV-IgG zuerst durch das 55 kDa-Antigen in Woche 3 und eine Woche später mit dem 3-2 (M)-Antigen nachgewiesen. Das SG3 (B)-Antigen wies keine Serokonvertierung in Cyno-395 nach und Anti-HEV-IgG wurde nur mit dem 55 kDa-Antigen nachgewiesen. Anti-HEV neigte dazu, sich im Titer mit der Zeit in diesem Tier zu verringern. - Cyno-380 und Cyno-383 wurden mit einer 10–3-Verdünnung der fäkalen Standard-Suspension von HEV inokuliert (Tabelle 5,
7E ,7F ,8C ). Cyno-380 wies fluktuierende ALT-Aktivitäten vor und nach Inokulation auf. Daher konnten ALT-Niveaus nicht zum Dokumentieren von Hepatitis E in diesem Tier verwendet werden. In Cyno-383 wurde ein leichter Anstieg an ALT-Aktivitäten beobachtet (7F ), der mit Serokonvertierung zusammenfiel und daher durch milde Hepatitis E bedingt sein könnte. Anti-HEV-IgM wurde nicht in Seren von Cyno-380 mit einem jeglichen der drei Antigene nachgewiesen. Cyno-380 serokonvertierte zu Anti-HEV-IgG, wenn er durch ELISA mit SG3 (B)- aber nicht mit 3-2 (M)-Antigen getestet wurde. Dieses Tier hatte vorher bestehendes Anti-HEV-IgG, wenn es mit dem 55 kDa-Antigen getestet wurde, aber es zeigte sich eine starke Erhöhung des Anti-HEV-IgGs ab Woche 5 (7E ). Identifizierung eines vorher bestehenden Antikörpers wurde schon früher in Seren aus einem anderen Cynomolgus-Affen berichtet [Ticehurst et al., (1992) J. Infect. Dis., 165: 835–845; Tsarev et al., (1993) J. Infect. Dis., 168: 369–378]. Serokonvertierung trat zum erwarteten Zeitpunkt auf, aber die Niveaus an Anti-HEV-IgG in Proben aus Cyno-383 blieben gering und nur mit dem 55 kDa-Antigen nachweisbar. - Cyno-389 und Cyno-393 wurden mit einer 10–4-Verdünnung der fäkalen Standardsuspension von HEV inokuliert (
7G ,7H ,8D , Tabelle 5). Keines der Tiere zeigte einen signifikanten Anstieg an ALT-Aktivitäten, obwohl der Zeitpunkt eines kleinen aber unterscheidbaren ALT-Peaks in Seren von Cyno-393 in Woche 5 (7H ) eine Hepatitis im Grenzbereich nahe legte. Ein ELISA, der auf den SG3 (B)- oder 3-2 (M)-Antigenen basierte, wertete beide Tiere als negativ für eine HEV-Infektion. Dagegen wies das 55 kDa-Antigen Anti-HEV-IgM in Seren von Cyno-389 bei Wochen 6 bis 8 nach Inokulation (8D ) und Anti-HEV-IgG von Woche 6 bis Woche 15 in beiden Tieren nach. - Kein Tier, das mit der 10–5-Verdünnung der fäkalen Standardsuspension inokuliert worden war, entwickelte eine erkennbare Erhöhung der ALT-Aktivitäten (
7I ,7J , Tabelle 5), aber in Cyno-386 wurden Anti-HEV-IgM und -IgG in Wochen 8 bis 13 bzw. 8 bis 15 mit dem 55 kDa-Antigen nachgewiesen (7J ,8E ). Anti-HEV-IgG in Cyno-385 wurde mit dem 55 kDa und dem 3-2 (M)-Antigen aber nicht mit dem SG3 (B)-Antigen nachgewiesen. Im Gegensatz zu vorherigen Muster wurde Anti-HEV-IgG mit einem Fusionsantigen vier Wochen früher und mit höheren Niveaus als mit dem 55 kDa-Antigen nachgewiesen. - Keines der Tiere, die mit Verdünnungen der fäkalen Standardsuspension von HEV im Bereich von 10–6–10–8 inokuliert worden waren, entwickelte einen Antikörper gegen ein jegliches der drei HEV-Antigene. Erhöhte ALT-Aktivitäten wurden in diesen Tieren mit Ausnahme eines eher deutlichen Peaks an ALT-Aktivität in Woche 9 in Cyno-400 (Tabelle 5) nicht beobachtet. Jedoch zeigte die Abwesenheit einer Sero konvertierung in diesem Tier, dass dieser Peak wahrscheinlich nicht durch eine HEV-Infektion bedingt war.
- In Bezug auf die zwei Cynomolgus-Affen (387 und 392), die mit der 10–1-Verdünnung der 10%igen fäkalen Suspension inokuliert worden waren, war keiner der Affen infiziert, da ALT-Niveaus nicht anstiegen und ein ELISA, der mit den 3-2 (M)- und 55 kDa-Antigenen durchgeführt wurde, keine Serokonvertierung zu HEV nachwies (Tabelle 5).
- Schließlich wurde ein serologischer Beweis für eine HEV-Infektion in allen Tieren gefunden, die mit dezimalen Verdünnungen der fäkalen Suspension bis 10–5 inokuliert worden waren. Keines der Tiere, die höhere Verdünnungen erhielten, zeigte solch einen Beweis. Bedeutende Hepatitis wie durch erhöhtes ALT definiert wurde nur in zwei Affen, die mit der 10–1-Verdünnung infiziert worden waren, beobachtet. Deutlich geringere Erhöhungen der ALT-Aktivitäten wurden in manchen Tieren, die mit höheren Verdünnungen der fäkalen Suspension inokuliert worden waren, beobachtet, während in anderen keine Erhöhungen gefunden wurden. Allein betrachtet waren diese geringen ALT-Erhöhungen nicht für Hepatitis diagnostisch. Jedoch legt das Zusammentreffen einer Serokonvertierung und eines Auftretens dieser ALT-Peaks das Vorliegen einer milden Hepatitis in diesen Tieren nah. Anti-HEV-IgG-Serokonvertierung wurde in allen Tieren nachgewiesen, die mit Verdünnungen der fäkalen Suspension von 10–1 bis 10–5 inokuliert worden waren. Eine Tendenz zu geringeren Niveaus an Anti-HEV-IgG und verzögerter Serokonvertierung wurde in Tieren beobachtet, die mit höheren Verdünnungen der Stammlösung inokuliert worden waren.
- Zusammengefasst war das Pakistani-55 kDa-ORF-2-Antigen wirksamer als entweder das 3-2 (M)- oder SG3 (B)-Antigen zum Nachweis von Anti-HEV-IgM und -IgG in Cynomolgus-Affen, die mit dem Pakistani-Stamm von HEV infiziert worden waren. Zum Beispiel war für alle Tierseren mit Ausnahme derer von Cyno-385 ein Nachweis von Anti-HEV-IgG oder -IgM durch ELISA mit dem 55 kDa-Antigen wirksamer als mit entweder dem 3-2 (M)- oder SG3-Antigen. ELISA mit dem 55 kDa-Antigen erzeugte intern konsistente und reproduzierbare Ergebnisse, wobei Anti-HEV-IgG in allen zehn Tieren nachgewiesen wurde, die mit einer fäkalen Verdünnung von 10–5 oder geringer inokuliert worden waren. Die Größenordnung der ELISA-Signale verringerte sich auch, wenn das Inokulum verdünnt wurde. Die Fusionsantigene erzeugten keine konsistenten Ergebnisse zwischen den Tierpaaren. Nur eines von je dem Tierpaar, das mit der 10–1-, 10–2-, 10–3- oder 10–5-Verdünnung inokuliert worden war, zeigte Serokonvertierung zu Anti-HEV-IgG und nur eine Serokonvertierung zu Anti-HEV-IgM wurde mit diesen Antigenen nachgewiesen. Keines der Tiere, die mit der 10–4-Verdünnung des Original-Inokulums inokuliert worden waren, serokonvertierte zu einem der beiden Fusionsantigene, obwohl Seren von einem Tier (Cyno-393) anhaltend hohe Niveaus an Anti-HEV-IgG zeigte, wenn es mit dem 55 kDa-Antigen untersucht wurde. Obwohl wie vorstehend diskutiert ELISA für Anti-HEV-IgM deutlich weniger sensitiv als ELISA für Cynomolgus-Anti-HEV-IgG war, war das 55 kDa-Antigen fähig, Anti-HEV-IgM in mehr Tieren nachzuweisen als das 3-2 (M)- oder SG3 (B)-Antigen. Zusammengefasst konnte keine endgültige Aussage über den infektiösen Titer des viralen Pakistani-Inokulums, das in dieser Studie verwendet wurde, mit den kombinierten Daten des 3-2 (M)- und SG3 (B)-basierten ELISA gemacht werden, aber sie konnte mit den Daten, die alleine mit dem 55 kDa Pakistani-ELISA erhalten wurden, gemacht werden.
- In Bezug auf Cyno-385 betrug der Unterschied im Anti-HEV-IgG-Nachweis zwischen den zwei Testergebnissen vier Wochen. Diese Daten legen die Anwesenheit eines unterschiedlichen Epitops im 3-2 (M)-Antigen, das durch dieses Tier erkannt wurde und das in den größeren 55 kDa- und SG3 (B)-Antigenen nicht vorhanden ist, nahe. Wenn ein Gesamt-Insektenzell-Lysat, das sowohl Gesamt-ORF2-(75 kDa) als auch 55 kDa-Proteine enthielt, als Antigen zum wiederholten Testen dieser Proben verwendet wurde, waren die Ergebnisse die gleichen wie wenn 55 kDa alleine verwendet wurde. Dieses Ergebnis legt nahe, dass dem 55 kDa-Protein nicht die Aminosäuren des 3-2-Epitops fehlen könnten, sondern dass die Konformation der 3-2-Epitopsequenz in allen drei in dieser Studie verwendeten Antigenen unterschiedlich ist. Schließlich ist es interessant zu bemerken, dass ungeachtet der Tatsache, dass das Antigen SG3 (B) einen längeren Teil von ORF-2 enthielt und die gesamte Sequenz des Epitops 3-2 umfasste, es nicht mehr positive Seren als das 3-2 (M)-Antigen nachwies.
- BEISPIEL 11
- Bestimmung des infektiösen Titers der viralen HEV-SAR-55-Stammlösung durch RT-PCR
- Eine Kenntnis des infektiösen Titers von Inokula ist für die Interpretation eines großen Teils der Daten, die in experimentellen Infektionen von Tiermodellen erhalten werden, kritisch. Jedoch ist bis jetzt der infektiöse Titer einer viralen HEV-Stamm lösung noch nicht berichtet worden. Zehnfache Verdünnungen der fäkalen Suspension, die den HEV-Stamm SAR-55 enthielt, wurden extrahiert und RT-PCR-Amplifikation wurde wie folgt zur Bestimmung der höchsten Verdünnung, in der HEV-Genome nachgewiesen werden konnten, durchgeführt. 200 µl fäkale Suspension wurde mit 0,4 ml 1,5 M NaCl plus 15% Polyethylenglykol (PEG) 8000 gemischt und über Nacht bei 4°C gelagert. Niederschläge wurden durch Zentrifugation für 3 Minuten in einer Mikrozentrifuge (Beckman, Palo Alto, CA) bei 16000 g gesammelt und in 475 µl einer Lösung, die 4,2 M Guanidinthiocyanat, 0,5% N-Lauroylsarcosin, 0,25 M IRIS-HCl (pH 8,0), 0,15 M Dithiothreitol (DTT) und 1,0 µg tRNA enthielt, gelöst. 50 µl 1 M IRIS-HCl (pH 8,0), 100 mM EDTA und 10% SDS wurden dann zugegeben. Die RNA wurde zweifach mit Phenol-Chloroform (1:1) bei 65°C gefolgt von Chloroform-Extraktion bei Raumtemperatur extrahiert. Zu der oberen Phase wurden 250 µl 7,5 M Ammoniumacetat gegeben und Nukleinsäuren wurden mit 0,6 ml 2-Propanol ausgefällt, mit 75% Ethanol gewaschen, mit 100% Ethanol gewaschen und für eine reverse Transkription (RT)-PCR verwendet.
- Zum Nachweis des HEV-Genoms wurden zwei Sätze an verschachtelten Primer, die Sequenzen von der 3'-Region (ORF-2) des SAR-55-Genoms darstellten, verwendet. Primer für reverse Transkription und die erste PCR sind als SEQ ID NO: 99: GTATAACGGATCCACATCTCCCCTTACCTC bzw. SEQ ID NO: 100: TACAGATCTATACAACTTAACAGTCGG gezeigt. Primer für die zweite PCR sind als SEQ ID NO: 101: GCGGCAGATCTCACCGACACCATTAGTAC bzw. SEQ ID NO: 102: TAACCTGGATCCTTATGCCGCCCCTCTTAG gezeigt. Der RNA-Niederschlag wurde in 20 µl 0,05 M Tris-HCl (pH 7,6), 0,06 M KCl, 0,01 M MgCl2, 0,001 M DTT, 40 Einheiten RNasin (Promega, Biotec, Madison, WI), 16 Einheiten reverse Transkriptase aus Vogel-Myeloblastose-Virus (Promega Biotec) und 10 pmol reverser Primer gelöst und eine Stunde bei 42°C inkubiert. Zu 20 µl des reverse Transkriptase-Gemisches wurden 100 µl 0,01 M Tris-HCl (pH 8,4), 0,05 M KCl, 0,0025 M MgCl2, 0,0002 M von jedem dNTP, 50 pmol direkter Primer, 50 pmol reverser Primer und vier Einheiten AmpliTaq (Perkin-Elmer Cetus, Norwalk, CT) unter 100 µl Leicht-Mineralöl gegeben. Die HEV-cDNA wurde durch 35 Zyklen PCR amplifiziert: eine Minute bei 94°C, eine Minute bei 55°C, eine Minute bei 72°C. Die Produkte der PCR wurden auf 1%igen Agarose-Gelen analysiert. Dann wurden 5 µl dieses Gemisches für die zweite Runde an Amplifikation unter den gleichen Bedingungen mit der Ausnahme, dass die Verlängerungszeit auf drei Minuten erhöht wurde, verwendet.
- Die RT-PCR-Produkte, die in allen Verdünnungen der Standard-HEV-Fäkalien im Bereich von 10–1 bis 10–5 (
9 ) hergestellt wurden, wurden auf einem 2%igen Agarosegel getrennt und wurden durch Ethidiumbromid-Färbung des Gels nachgewiesen. Eine Verringerung der Menge des spezifischen PCR-Produkts bei höheren Verdünnungen wurde beobachtet und die höchste Verdünnung der 10%igen fäkalen Suspension, bei der das HEV-Genom nachgewiesen wurde, war 10–5. Daher war in Anbetracht des Verdünnungsfaktors der HEV-Genomtiter ungefähr 106,7 pro Gramm Fäkalien. - Zusätzlich waren nur diejenigen Verdünnungen, für die durch RT-PCR gezeigt wurde, dass sie das HEV-Genom enthalten, infektiös für Cynomolgus-Affen. Daher waren der Infektionstiter der fäkalen Standardsuspension und ihr Genomtiter wie durch RT-PCR nachgewiesen ungefähr gleich. Eine ähnliche Korrelation zwischen RT-PCR- und Infektivitätstiter wurde für einen Stamm von Hepatitis C-Virus gefunden [Cristiano et al., (1991) Hepatology, 14: 51–55; Farci et al., (1991) N. Engl. J. Med., 25: 98–104; Bukh et al. (1992); Proc. Natl. Acad. Sci. U.S.A., 89: 187–191].
- BEISPIEL 12
- Aktive Immunisierung unter Verwendung des ORF-2-Proteins als ein Vakzin und passive Immunisierung mit Anti-HEV positivem Rekonvaleszentenplasma
- Cynomolgus-Affen (Macaca fascicularis), die negativ (< 1:10) für HEV-Antikörper in einem ELISA waren, der auf dem 55 kDa ORF-2-Protein basierte, wurden einzeln unter Eingrenzung des biologischen Risikos gemäß BL-2 gehalten und eine Suspension (in fötalem Rinderserum) an Fäkalien, die den Pakistani-HEV-Stamm SAR-55 enthielten und so verdünnt waren, dass sie 10000 oder 1000 CID50 enthielten, wurde zur intravenösen Inokulation von Tieren verwendet.
- Für Studien der aktiven Immunisierung wurde 55 kDa ORF-2-Protein, das rekombinant mittels Baculovirus exprimiert wurde, aus 5 × 108 SF-9-Zellen, die sieben Tage nach Inokulation geerntet wurden, wie in Beispiel 10 beschrieben, gereinigt. 3 mg des gereinigten 55 kDa-Proteins wurden mit Alaun ausgefällt und acht Cynomolgus-Affen wurden durch intramuskuläre Injektion mit 0,5 ml Vakzin, das 50 µg des Alaun-ausgefällten 55 kDa-Proteins enthielt, immunisiert. Vier Affen erhielten eine einfache Dosis und vier Affen erhielten vier Wochen voneinander getrennt zwei Dosen. Primaten wurden intravenös mit 1000–10000 CID50 an HEV vier Wochen nach der letzten Immunisierung belastet.
- Vier Cynomolgus-Affen dienten in den Studien der aktiven Immunisierung als Kontrolle. Cyno-412 und -413 erhielten eine Dosis Placebo (0,5 ml Phosphat-gepufferte Kochsalzlösung) und Cyno-397 und -849 erhielten zwei Dosen Placebo. Die Kontrolltiere wurden mit 1000–10000 CID50 an HEV belastet.
- Für Studien der passiven Immunität wurde Cyno-384 mit 0,5 ml einer 10%igen vereinigten Stuhlsuspension, die zwei chinesische HEV-Isolate, KS1-1987 und KS2-1987, enthielt, infiziert und Plasma wurde wiederholt von dem Tier während der Genesung gesammelt (Yin et al. (1993) J. Med. Virol., 41: 230–241). Ungefähr 1% des Bluts von Cyno-396 und Cyno-399 und 10% des Bluts von Cyno-401 und Cyno-402 wurde mit Rekonvaleszentenplasma aus Cyno-384 mit einem HEV-Antikörpertiter von 1:10000 ersetzt. Tiere wurden mit 1000 CID50 an HEV zwei Tage nach Infusion des Plasmas belastet. Als Kontrolle wurden 10% des Bluts von Cyno-405 mit Anti-HEV-negativem Plasma ersetzt, das von Cyno-384 vor Infektion mit HEV erhalten wurde. Cyno-405 wurde dann mit 1000 CID50 an HEV belastet.
- Für die Studien sowohl der passiven als auch der aktiven Immunisierung wurden perkutane Nadelbiopsien der Leber und Proben an Serum und Fäkalien vor Inokulation und wöchentlich für 15 Wochen nach Inokulation gesammelt. Seren wurden auf Alanin-Aminotransferase (ALT)-Niveaus mit kommerziell erhältlichen Tests (Metpath Inc., Rockville, MD) untersucht und ein biochemischer Nachweis von Hepatitis wurde als eine zweifache oder größere Erhöhung an ALT definiert. Leberbiopsien wurden kodiert untersucht und der verwendete Anti-HEV-ELISA wurde in Beispiel 10 beschrieben. RNA-Extraktion und RT-PCR wurden wie in Beispiel 11 durchgeführt, mit der Ausnahme, dass RNA aus 100 µl Serum oder aus 100 µl 10%iger fäkaler Suspension mit TRlzol-Reagenz (Gibco BRL, Gaithersburg, Maryland) gemäß dem Protokoll des Herstellers extrahiert wurde. Zur Quantifizierung wurden PCR-positive serielle Seren oder Fäkalien von jedem Tier vereinigt und seriell in zehnfachen Schritten in Kälberserum verdünnt. 100 µl jeder Verdünnung wurden zur RNA-Extraktion und für RT-PCR wie vorher in diesem Beispiel beschrieben verwendet. Das in dieser Studie verwendete PCR-Protokoll konnte so wenig wie 10 CID50 an HEV pro ml Serum und so wenig wie 100 CID50 pro Gramm Fäkalien nachweisen.
- Peak-ALT-Werte von wöchentlichen Serumproben für 5 Wochen vor Inokulation und für 15 Wochen nach Inokulation wurden als Verhältnisse (nach/vor) für jedes Tier angegeben. Das geometrische Mittel der Verhältnisse der Kontrollgruppe an Tieren wurde mit dem von den passiv oder aktiv immunisierten Tieren unter Verwendung des Simes-Tests (Simes, R. J. (1986) Biometrika, 73: 751–754) verglichen.
- Die Dauer an Virämie und Virusabgabe in Fäkalien und die HEV-Genomtiter in der Kontrollgruppe an Tieren wurden mit denen in passiv oder aktiv immunisierten Tieren unter Verwendung des Wilcoxon-Tests [Noether, G. (1967) in Elements of nonparametric statistics (John Wiley and Sons Inc., New York), Seiten 31–36.] verglichen. Der gleiche Test wurde verwendet, um die vorstehenden Parameter zwischen passiv und aktiv immunisierten Tieren zu vergleichen.
- Für eine statistische Analyse wurden Serumproben, die < 10 HEV-Genome in 1 ml Serum aufwiesen, ein Titer von 1:1 zugewiesen und fäkalen Proben, die < 100 HEV-Genome in 1 g Fäkalien aufwiesen, wurde ein Titer von 1:10 zugewiesen.
- ERGEBNISSE
- Verlauf einer Hepatitis E-Infektion in nicht-immunisierten Tieren.
- In drei von fünf nicht-immunisierten Tieren, die mit HEV belastet worden waren, wurde ein biochemischer Nachweis von Hepatitis durch eine mindestens zweifache Erhöhung der Serum-ALT-Werte dokumentiert. In zwei Tieren wurden keine signifikanten Erhöhungen der ALT-Aktivität gefunden. Jedoch dokumentierten histopathologische Daten Hepatitis in allen fünf Tieren wie in Tabelle 6 gezeigt.
- Nekrose-Entzündungs-Änderungen lagen zwischen 1+ und 2+ auf einer Skala von 1+ bis 4+ und waren zeitlich mit Erhöhungen von ALT-Aktivitäten in denjenigen Tieren mit solchen Erhöhungen assoziiert.
- Alle Kontrolltiere serokonvertierten zu HEV drei bis fünf Wochen nach Belastung und entwickelten maximale HEV-Antikörpertiter von 1:1000 bis 1:32000. Es gab eine gute Korrelation zwischen der Schwere einer Infektion, Hepatitis, und dem Niveau an Anti-HEV-Antwort. Cyno-405, der den höchsten kumulativen Wert für Hepatitis aufwies, wies auch die längste Zeitspanne an Virämie und viraler Exkretion und das höchste Niveau an Anti-HEV auf (Tabelle 6). Die Dauer der viralen Absonderung in Fäkalien war die gleiche wie oder länger als die der Virämie. Für alle Kontrolltiere waren die Titer des HEV-Genoms im Serum geringer (10–3 bis 10–4,7) als die Titer in Fäkalien (10–5,7 bis 10–7). In allen fünf dieser Tiere wurde Virämie und Virusabsonderung in Fäkalien für vier bis elf Wochen und für einen Durchschnitt von 4,2 Wochen nach Serokonvertierung (Bereich 2–9 Wochen) nachgewiesen.
- Passive Immunisierung. Cyno-396 und -399, bei denen ungefähr 1% ihres Bluts durch Anti-HEV-positives Rekonvaleszentenplasma ersetzt worden war, wiesen einen HEV-Antikörpertiter von 1:40 auf, wenn dieser zwei Tage nach Transfusion (zum Zeitpunkt der Belastung) bestimmt wurde (Tabelle 6). Eine zweifache Verringerung des HEV-Antikörpertiters wurde in beiden Tieren eine Woche nach Transfusion beobachtet und HEV-Antikörper verringerten sich unter das nachweisbare Niveau (< 1:10) zwei Wochen nach Transfusion. Anti-HEV wurde wieder fünf Wochen nach Belastung in Cyno-396 und vier Wochen nach Belastung in Cyno-399 nachgewiesen, was zeigte, dass eine Infektion mit HEV erfolgt war. Der maximale HEV-Antikörpertiter (1:8000) wurde 9–10 Wochen nach Belastung erreicht. Kein Cynomolgus-Affe zeigte einen signifikanten Anstieg an ALT-Aktivität nach Belastung. Jedoch wurden histologische Anzeichen für Hepatitis in Cyno-396 nachgewiesen und das HEV-Genom wurde in Serum und Fäkalien von beiden Tieren nachgewiesen (Tabelle 6).
- Cyno-401 und -402 hatten etwa 10% ihres Blutes durch Rekonvaleszentenplasma ersetzt. Zwei Tage nach Transfusion, zum Zeitpunkt der Belastung, lag der HEV-Antikörpertiter in beiden Cynomolgus-Affen bei 1:200 (Tabelle 7).
- Anti-HEV wurde durchgehend in beiden Tieren während der 15 Wochen nach Belastung nachgewiesen und erreichte einen maximalen Titer von 1:4000 in Cyno-401 aber nur 1:80 in Cyno-402. Biochemische und histologische Analysen zeigten keine Hepatitis in beiden Tieren. Jedoch wurden in beiden Tieren HEV-Virämie und fäkales Absondern von Virus beobachtet, was zeigt, dass eine Infektion stattgefunden hatte (Tabelle 6). Folglich schützte passive Immunprophylaxe, die einen höheren Titer an Antikörper erreichte, Cynomolgus-Affen gegen Hepatitis nach Belastung mit HEV.
- Aktive Immunisierung. Vier Primaten, die mit einer 50 µg-Dosis des 55 kDa-Proteins immunisiert worden waren, entwickelten Antikörper gegen das rekombinante Protein mit einem Titer von 1:100 bis 1:10000 (Tabelle 7). Einer (Cyno-013) starb durch einen Anästhesieunfall neun Wochen nach Belastung und wird in den Analysen eingeschlossen (Tabelle 6). Die vier Tiere, die zwei Dosen des Antigens erhielten, entwickelten HEV-Antikörper mit Titer von 1:10000. Zwei der vier Affen starben in Folge intravenöser Belastung mit HEV. Dies könnte auch das Ergebnis eines Anästhesieunfalls sein, aber die genaue Ethyologie konnte nicht bestimmt werden. Diese zwei Affen wurden von weiteren Analysen ausgeschlossen. Keines der sechs verbliebenen Tiere entwickelte abnormale ALT-Niveaus oder histologische Anzeichen für Hepatitis nach Belastung (Tabelle 6). Cynomolgus-Affen, die mit entweder ein oder zwei Dosen des 55 kDa-Proteins immunisiert worden waren, entwickelten keine Virämie. Jedoch sonderten drei von vier Tieren, die eine Dosis des Immunogens erhalten hatten, Virus in ihre Fäkalien ab. Im Gegensatz dazu wurde keine Virusabsonderung in den beiden belasteten Tieren beobachtet, die zwei Dosen des Vakzins erhalten hatten.
- Die meisten der aktiv immunisierten Tiere entwickelten höhere HEV-Antikörpertiter als die passiv immunisierten Tiere. Jedoch wies Cyno-013 einen HEV-Antikörpertiter von 1:100 zum Zeitpunkt der Belastung verglichen mit einem Titer von 1–200 in zwei Tieren, die passiv mit Anti-HEV-Plasma immunisiert worden waren, auf. Cyno-013 zeigte jedoch einen größeren Schutz gegen HEV-Infektion als die passiv immunisierten Tiere. Cyno-009, der einen HEV-Antikörpertiter von 1:1000 zum Zeitpunkt der Belastung aufwies, war komplett gegen Hepatitis und HEV-Infektion geschützt (Tabelle 6). Im Gegensatz dazu wurde Cyno-003 infiziert und sonderte HEV in Fäkalien ab, obwohl er einen HEV-Antikörpertiter von 1:1000 zum Zeitpunkt der Belastung aufwies. Jedoch wurde weder Hepatitis noch Virämie in diesem Tier oder in anderen Cynomolgus-Affen, die eine Dosis Immunogen erhielten und HEV-Antikörpertiter von 1:10000 oder größer aufwiesen, nachgewiesen.
- Vergleich des Verlaufs einer HEV-Infektion in Kontroll- und immunisierten Tieren.
- Wie durch Histopathologie gemessen waren alle immunisierten Tiere mit Ausnahme von einem der passiv immunisierten Affen gegen Hepatitis nach intravenöser Belastung mit HEV geschützt. Vergleich von Durchschnittswerten für die Schwere der Hepatitis und das Niveau einer viralen Replikation zwischen der Kontrollgruppe und den passiv und aktiv immunisierten Tieren zeigte, dass im Allgemeinen die Schwere der Infektion invers mit dem HEV-Antikörpertiter zum Zeitpunkt der Belastung zusammenhing und sich in der Reihenfolge: nicht immunisiert > passive Immunisierung (1%) > passive Immunisierung (10%) > aktive Immunisierung (1 Dosis) > aktive Immunisierung (2 Dosen) verringerte (Tabellen 6, 8). Jedoch war die Anzahl an Tieren in jeder der zwei Untergruppen von passiv und aktiv immunisierten Tieren nicht ausreichend, um eine statistische Analyse zu erlauben. Daher wurde eine statistische Analyse für kombinierte passiv immunisierte bzw. kombinierte aktiv immunisierte Gruppen im Vergleich mit den kombinierten Kontrollgruppen durchgeführt. Die Ergebnisse dieser Analyse sind in Tabelle 8 dargestellt.
- Sie zeigen, dass die histopathologischen Werte und Dauer der histologischen Veränderungen in der Kontrollgruppe statistisch unterschiedlich zu denen der passiv oder aktiv immunisierten Tiere waren. Die höheren Verhältnisse der Peak-ALT-Werte vor/nach Inokulation in der Kontrollgruppe waren statistisch signifikant, wenn sie mit denjenigen der passiv oder aktiv immunisierten Tiere verglichen wurden, was einen Schutz gegen biochemische Manifestationen von Hepatitis in beiden Gruppen an immunisierten Tieren anzeigt. Die Dauer an Virämie und der HEV-Titer in den Fäkalien waren in beiden Gruppen an immunisierten Tieren deutlich niedriger als in der Kontrollgruppe. Unterschiede in der Dauer an Virusabsonderung und HEV-Titer in Serum waren jedoch zwischen der Kontrollgruppe und der passiv immunisierten Gruppe nicht statistisch unterschiedlich, obwohl diese Parameter deutlich unterschiedlich waren, wenn die Kontrollgruppe mit der aktiv immunisierten Gruppe verglichen wurde. Deutliche Unterschiede wurden auch zwischen passiv und aktiv immunisierten Gruppen an Tieren für die Dauer einer Virämie und eines fäkalen Absonderns sowie für HEV-Titer gefunden.
- Zusammengefasst zeigen die in Tabellen 6–8 gezeigten Ergebnisse, dass sowohl passiv als auch aktiv erworbene HEV-Antikörper Cynomolgus-Affen gegen Hepatitis nach einer Belastung mit virulentem HEV schützten. Obwohl alle fünf nicht immunisierten Cynomolgus-Affen histologische Anzeichen für Hepatitis entwickelten, wenn sie mit 1000–10000 CID50 an SAR-55 belastet worden waren, waren beide Tiere mit passiv erworbenen Antikörpertitern von 1:200 vor Hepatitis geschützt und eines von zwei Tieren mit einem Antikörpertiter von nur 1:40 entwickelte auch keine Hepatitis.
- Jedoch sollte bemerkt werden, dass aktiv immunisierte Tiere einen kompletten Schutz gegen Hepatitis und wirksamere Resistenz gegen HEV-Infektion als passiv immunisierte Tiere zeigten. Zum Beispiel wurde im Gegensatz zu Ergebnissen, die von den passiv immunisierten Tieren erhalten wurden, keine Virämie in aktiv immunisierten Tieren nach Belastung mit HEV nachgewiesen. Ein HEV-Antikörpertiter mit einer Höhe von so hoch wie 1:10000 konnte in Cynomolgus-Affen nach einer oder zwei Immunisierungen mit dem rekombinanten 55 kDa-Protein erreicht werden. Obwohl ein Affe (013) einen Titer von 1:100 nach aktiver Immunisierung entwickelte, verhinderte dieses Niveau immer noch Hepatitis und Virämie.
- Die Studien der aktiven Immunisierung zeigten auch, dass, während eine einzige Dosis Vakzin HEV-Virämie verhinderte, virale Abscheidung in Fäkalien immer noch nachzuweisen war. Jedoch wurde beobachtet, dass zwei Dosen Vakzin alle Anzeichen einer Hepatitis und HEV-Infektion verhinderten. Diese Ergebnisse legen daher nahe, dass eine einzelne Dosis Vakzin, die z. B. Individuen vor einer Auslandsreise verabreicht wird, diese vor Hepatitis E in Hochrisikoumgebungen schützen würde.
- Schließlich ist zu bemerken, dass die gezeigten Ergebnisse sehr ähnlich zu Ergebnissen sind, die vorher für passive und aktive Immunprophylaxe von nicht-menschlichen Primaten gegen Hepatitis A berichtet worden sind: passive Immunprophylaxe verhinderte Hepatitis aber nicht Infektion, wohingegen Vakzinierung nicht nur Hepatitis sondern auch Infektion mit HAV verhinderte (Purcell, R. H. et al. (1992) Vaccine, 10: 5148–5149). Es ist von Interesse, dass die hierin gezeigte Studie der Immunprophylaxe gegen HEV der vorherigen Studie der Immunprophylaxe gegen HAV sowohl bei Bestimmung des Antikörpertiters, der schützte (< 1:100), als auch im Ergebnis nach intravenöser Belastung mit virulentem Virus entspricht. Da andere Studien eine Wirksamkeit von vergleichbaren Titern an passiv und aktiv erhaltenem Anti-HAV in Menschen zeigten und den Vorhersagewert von Studien an Primaten in der Hepatitisforschung bestätigt haben (Stapleton, J. et al. (1985) Gastroenterology 89: 637–642; Inns, B. L. et al. (1992) Vaccine, 10: S159), ist es daher sehr wahrscheinlich, dass diese Ergebnisse in Cynomolgus-Affen eine Vorhersage für einen Schutz in Menschen sein werden.
- BEISPIEL 13
- Direkte Expression von gesamtem ORF-2 Protein und Fragmenten geringeren Molekulargewichts in Hefe
- Vier cDNA-ORF-2-Fragmente, die für:
- 1. gesamtes ORF-2-Protein (AS 1–660, MW 70979), Fragment 1778–1703. (wobei die Fragmentnummern sich auf die nachstehend angegebenen Primernummern beziehen)
- 2. ORF-2-Protein, das von der 34. AS startet, (AS 34–660, MW 67206), Fragment 1779–1703.
- 3. ORF-2-Protein, das von der 96. AS startet (AS 96–660, MW 60782), Fragment 1780–1703.
- 4. ORF-2-Protein, das von der 124. AS startet (AS 124–660, MW 58050), Fragment 1781–1703.
- Alle in SEQ ID NOs: 103–107 gezeigten Sequenzen enthalten die künstliche Sequenz CCTAGG an ihren 5'-Enden, die von vier Nukleotiden angeführt wird. Die künstliche Sequenz war eine Erkennungsstelle für das Restriktionsenzym AvrII (BlnI). Synthetische PCR-Fragmente wurden mit BlnI geschnitten und in die AvrII-Stelle des pPIC9-Vektors (
10 ) (Invitrogen) kloniert. Korrekte Orientierung der Fragmente wurde durch Restriktionsanalyse unter Verwendung asymmetrischer EcoRI-Stellen, die in ORF-2-Sequenzen und im Vektor vorhanden sind, bestätigt. Gereinigte rekombinante Plasmide pPIC9-1778 (enthaltend Fragment 1778–1703), pPIC9-1779 (enthaltend Fragment 1779–1703), pPIC9-1780 (enthaltend Fragment 1780–1703) und pPIC9-1781 (enthaltend Fragment 1781–1730) wurden zur Transformation von Hefespheroplast (Picha-Stamm) gemäß dem Invitrogen-Protokoll verwendet. Screenen von rekombinanten Klonen und Analyse der Expression wurden unter Verwendung des gleichen Protokolls durchgeführt. Diese exprimierten Proteine können als Immunogene in Vakzinen und als Antigene in Immunoassays wie in der vorliegenden Anmeldung beschrieben verwendet werden. Schließlich würde der Fachmann erkennen, dass der Vektor und Hefestamm, die in dem vorstehenden Beispiel verwendet wurden, durch andere Vektoren (z. B. pHIL-F1; Invitrogen) oder Hefestämme (z. B. Saccharomyces Cerevisiae) ersetzt werden könnten. - BEISPIEL 14
- Reinigung und aminoterminale Sequenzanalyse von HEV-ORF-2-Genprodukten, die in SF-9-Insektenzellen infiziert mit rekombinantem Baculovirus 63-2-IV-2 synthetisiert wurden
- Wie in Beispiel 10 beschrieben wurden SF-9-Zellen mit rekombinantem Baculovirus 63-2-IV-2 infiziert und sieben Tage nach Inokulation geerntet. Die vorherrschende Proteinbande, die auf einem SDS-PAGE des Insektenzell-Lysats vorhanden war, hatte ein Molekulargewicht von etwa 55 kDa. Weitere Reinigung dieser 55 kDa-Bande wurde durch Ionenaustauscher-Säulenchromatographie unter Verwendung von DEAE-Sepharose mit einem 150–450 mM NaCl-Gradienten erreicht. DEAE-Fraktionen wurden auf die Anwesenheit der 55 kDa-Bande durch SDS-PAGE gefolgt von Coomassie-Blau-Färbung untersucht. Die Peak-Fraktion wurde dann durch Polyacrylamid-Gelelektrophorese in Abwesenheit von SDS in drei Banden von 55 kDa, 61 kDa und eine Bande von dazwischen liegendem Molekulargewicht aufgelöst. Analyse jeder Proteinbande vom Polyacrylamidgel durch aminoterminales Mikroprotein-Sequenzieren zeigte, dass die 55 und 61 kDa-Proteine einen einzigartigen N-Terminus bei Ala-112 von SEQ ID NO: 2 teilten. Es wird angenommen, dass die Größendifferenzen bei den zwei ORF-2-Spaltprodukten jeweils unterschiedliche COOH-terminale Spaltung des größeren Produkts widerspiegeln können.
- Es wurde gezeigt, dass das dritte dazwischen liegende Protein auf dem Polyacrylamidgel ein Baculovirus-Chitinase-Protein war. Die 55 und 61 kDa ORF-2-Proteine wurden in eine einzelne symmetrische Peak-Fraktion, die frei von Chitinase war, durch Durchführung einer reverse Phase-HPLC unter Verwendung eines Mikroporensystems mit NaCl- und Acetonitril-Lösungsmitteln mit den Peak-DEAE-Fraktionen aufgelöst.
- BEISPIEL 15
- Direkte Expression der 55 und 61 kDa-Spaltprodukte
- Ein cDNA-ORF-2-Fragment, das für ein ORF-2-Protein kodiert, das bei der 112. Aminosäure startet (Aminosäuren 112–660 von ORF-2), wurde mittels PCR unter Verwendung des Plasmids p63-2 als die Matrize erhalten. Das cDNA-Fragment wurde dann in einen pBlueBac-3-Transfervektor an der BamHI-PstI-Stelle im Vektor inseriert. SF9-Insektenzellen werden mit dem rekombinanten Baculovirus, der von diesem Vektor erstellt wurde, infiziert und Insektenzell-Lysate werden auf Anwesenheit der 55 und 61 kDa-ORF-2-Proteine durch Coomassie-Blau-Färbung von Polyacrylamidgelen analysiert. Das/die direkt exprimierte(n) Protein(e) kann/können als Immunogene in Vakzinen und als Antigene in Immunoassays wie hierin beschrieben verwendet werden.
- BEISPIEL 16
- Kinetik der HEV-ORF-2-Proteinexpression in Insektenzellen
- Die Expressionskinetik und Reinigung von Volllängen- und verkürzten Versionen des HEV-ORF2 (Pakistani-Stamm) in Baculovirus-infizierten Insektenzellen wurden untersucht. Die in diesem Beispiel beschriebenen 72 und 63 kDa ORF2-Proteine sind die gleichen Proteine wie die 74 und 61 kDa-Proteine, die hierin vorher in Beispielen 3 bzw. 14 beschrieben wurden. Der Unterschied in den Molekulargewichten fällt in den kleinen Bereich der normalen Variabilität, die für eine Bestimmung von Molekulargewichten durch Mobilität in Gelelektrophorese beobachtet wird.
- Zellkultur. Spodoptera frugiperda-Zellen, Klon 9 (Sf-9), wurden als Monolager-Kulturen für Plaque-Assays und Transfektionen und als Schüttler-Suspensionskulturen für Virusinfektionen zum Herstellen von Hoch-Titer-Virusstammlösungen und rekombinantem Protein kultiviert. SF-9-Zellen wurden bei 28°C und 150 UpM in Sf-900 II-serumfreiem Medium (SFM) (Life Technologies, Inc., Gaithersburg, MD) in Trockenluft-Inkubatoren gehalten und wurden von einer Startdichte von 0,2 × 106 Zellen/ml auf eine Enddichte von 1,0 × 107 Zellen/ml als Suspensionskulturen bis zu Passage 70 subkultiviert.
- Virusinfektionen. Rekombinante Autographs californica multinukleare Polyhedrose-Baculoviren (AcMNPV) wurden in Sf-9-Zellen (2,0 × 106 Zellen/ml) bei einer geringen Multiplizität der Infektion (MOI; 0,01) passagiert. Virusinfektionen zum Zwecke der rekombinanten Proteinproduktion wurden bei einer MOI = 5 gestartet und vier Tage gehalten, bis eine Überlebensrate < 10% erreicht wurde. Plaque-Agaroseassays wurden in 6-Näpfchen-Platten mit Sf-9-Zellmonolayern bei 75% Konfluenz durch Standardverfahren durchgeführt.
- Konstruktion von rekombinanten Baculoviren. Rekombinante Baculoviren (
11 ), die Volllängen-(bHEV ORF2 fl) und eine 5' verkürzte Deletion (bHEV ORF2 5' tr) von HEV-ORF2 (Pakistani-Stamm) enthielten, wurden durch Standardhomologe Rekombination in Sf-9-Insektenzellen konstruiert. Ein rekombinanter Baculovirus, der eine 5'-3'-Verkürzungsdeletion von HEV-ORF2 enthielt, wurde unter Verwendung von Bacmid-Vektoren (Luckow, V. A. et al. (1993) J. Virol. 67: 4566–4579) wie folgt konstruiert:
Oligonukleotidprimer HEV-140 (5'-TTCGGATCCATGGCGGTCGCTCCGGCC-3') (SEQ ID NO: 108) und HEV-141 (5'-TCAAGCTTATCATCATAGCACAGAGTGGGGGGC-3') (SEQ ID NO: 109) wurden zum Klonieren eines 1512 bp PCR-erstellten DNA-Fragments, das Aminosäuren 112–607 von HEV-ORF2 mit seinem eigenen ATG-Translationsinitiationscodon und multiplen Stoppcodons kodiert, von p61.2 in pCR2.1 (InVitrogen, San Diego, CA) durch T/A-PCR-Klonierung verwendet. Ein 1520 bp BamH-EcoRI-DNA-Fragment, das HEV-ORF2-DNA-Sequenzen enthielt, wurde stromabwärts des polh-Promotors innerhalb des polh-Lokus in das Baculovirus-Donorplasmid pFASTBAC-1 (Life Technologies, Inc.) inseriert. Rekombinante Baculoviren, die die HEV-ORF2-DNA enthielten, wurden von Sf-9-Zellen, die mit der rekombinanten Bacmid-DNA unter Verwendung des kationischen Lipids CELLFECTIN (Life Technologies, Inc.) transfiziert waren, isoliert. Plaque-gereinigte Virusisolate wurden auf Integrität des HEV-ORF2-DNA-Inserts und Proteinexpression in Insektenzellen gescreent und in einer Mastervirus-Saatbank, die bHEV-ORF2 5'-3'-tr-Virus genannt wurde, expandiert. - Prozessierung von infizierten Zellen und Überstand. Infizierte Zellen und Überstandsmedien wurden zu angegebenen Zeitpunkten durch Zentrifugation bei 500 × g und 4°C für 5 Minuten geerntet und auf rekombinante HEV-ORF2-Proteine prozessiert. Zell-Lysate wurden durch Resuspendierung von Zellniederschlägen in Lyse-Puffer (0,5% NP-40, 50 mM Tris-HCl, pH 8,0, 2 mM EDTA) bei 2 ml pro mg Zellniederschlag hergestellt und mit frischem Aprotinin auf eine Endkonzentration von 2 mg/ml ergänzt, kurz gevortext und 20 Minuten auf Eis inkubiert. Zellkerne wurden durch Niedriggeschwindigkeitszentrifugation bei 3000 × g und 4°C für 15 Minuten sedimentiert und die cytoplasmatische Fraktion wurde gesammelt und als Zell-Rohlysat verwendet. Die Überstände infizierter Zellen und Zell-Lysate wurden durch Zentrifugation bei 12000 × g und 4°C für 60 Minuten unter Verwendung des Sorvall SS34-Rotors geklärt.
- Reinigung von HEV-ORF2-Proteinprodukten. Rekombinante HEV-ORF2-Proteine wurden von geklärten Lysaten und Überstandsmedien von Baculovirus-infizierten Zellen getrennt voneinander gereinigt. Das Zell-Rohysat wurde 1:10 mit Beladungspuffer (50 mM Tris-HCl, pH 8,0, 10 mM NaCl) verdünnt.
- Geklärte Überstände infizierter Zellen wurden zehnfach durch Tangentialfluss-Ul-trafiltration unter Verwendung eines spiralgewundenen Cellulose-Ultrafiltrationseinsatzes (S1Y10; 1 Sq. Ft. Fläche; 10000 MW Cutoff; Amicon, Beverly, MA) auf ei nem Amicon Proflux M-12 Ultrafiltrationssystem bei einer Rezirkulationsrate von 4 l/Minute und einem Transmembrandruck von 20 PSI konzentriert. Der konzentrierte Überstand wurde gegen 4 Volumen Beladungspuffer diafiltriert.
- Das Diafiltrat oder verdünnte Rohlysat (1,5 Bettvolumen) wurde auf eine Q-Sepharose Fast Flow starker Anionenaustauscher-Säule (XK50-Säule, 5,0 × 7,5 cm, 150 ml; Pharmacia, Piscataway, NJ) bei einer Flussrate von 5,0 ml/Minute geladen. Die Säule wurde zuerst mit 1,0 Bettvolumen Beladungspuffer bei einer Flussrate von 5 ml/Minute gefolgt von einem zweiten Waschschritt mit 1,0 Bettvolumen Beladungspuffer bei einer Flussrate von 20 ml/Minute gewaschen. Die Proteine wurden mit 6,5 Bettvolumen eines kontinuierlichen linearen Gradienten an NaCl von 10–300 mM im gleichen Puffer bei einer Flussrate von 20 ml/Minute eluiert.
- 10 µl-Aliquots von Q-Sepharose-Säule (Pharmacia, Piscataway, NJ)-Peak-Proteinfraktionen wurden einer SDS-PAGE-Analyse zur Identifizierung von HEV-ORF2 (+) Proteinfraktionen unterworfen. Zusammengeführte (+)-Fraktionen wurden durch Gelfiltration unter Verwendung von Sepharose G-25 (Pharmacia) und Beladungspuffer entsalzt. Die Peak-Proteinfraktion wurde gesammelt und auf eine Source 15 Q High Performance (Pharmacia) starker Anionenaustauscher-Säule zum Trennen von HEV-ORF2-Polypeptiden geladen. Die Säule wurde wie vorstehend für Q-Sepharose-Flüssigchromatographie beschrieben gewaschen und eluiert. Zusammengeführte HEV-ORF2-Protein (+)-Fraktionen wurden wie vorstehend identifiziert, zusammengeführt und einer abschließenden Gelfiltration auf einer Sephacryl S-200-Säule (Pharmacia) unter Verwendung von Beladungspuffer für eine abschließende Proteinreinigung unterworfen. HEV-ORF2-Proteinfraktionen wurden durch SDS-PAGE- und Western Blot-Analysen wie nachstehend beschrieben identifiziert.
- Proteinkonzentrationen wurden durch den BCA/Pierce-Mikroproteinassay bei 60°C unter Verwendung von Rinderserumalbumin als ein Proteinstandard bestimmt. Die gesamte Chromatographie wurde unter Verwendung eines Waters 600E-Chromatographie-Arbeitsplatzsystems (Medford, MA) durchgeführt, das mit Millennium 2010-Software zum Steuern und Überwachen des Prozesses ausgestattet war. Puffer-Leitfähigkeiten wurden unter Verwendung eines AccuMet 20-Leitfähigkeitsmessgeräts bestimmt. Ein Corning 220 pH-Messgerät wurde für Bestimmungen von Puffer-pH-Werten verwendet. Alle Pufferkomponenten waren Rohmaterialien von USP- oder Molekularbiologie-Qualität.
- SDS-PAGE- und Western Blot-Analysen. Proteine wurden zweifach in Proteindenaturierungsprobenpuffer (126 mM Tris-HCl, pH 6,8, 5% β-Mercaptoethanol, 20% Glycerin, 2% SDS und 0,005% Bromphenolblau) verdünnt und bei 99°C 5 Minuten denaturiert. Denaturierte Proben wurden auf 8-16%igen Gradienten-SDS-Polyacrylamid-Gelen (NOVEX) elektrophoretisch getrennt (Laemmli, U. K. et al. (1970) Nature 227: 680–685). Proteine wurden durch Färbung von Proteingelen mit kolloidaler Coomassie-Blau-Färbelösung (NOVEX, San Diego, CA) wie durch den Hersteller vorgeschlagen sichtbar gemacht.
- Proteine wurden auf PVDF-Membranen durch Elektroblot-Techniken transferiert (Tsarev, S. A. et al. (1993) J. inf. Dis. 168: 369–378). HEV-ORF2-Produkte wurden chromogen durch Bindung an primäre Antiseren (polyklonaler α-HEV aus Schimpanse; 1:500) gefolgt von Bindung an sekundäre Antiseren (Ziege-α-Mensch-IgG2 konjugiert an alkalische Phosphatase; 1:5000; Life Technologies, Inc.) nachgewiesen. NBT/BCIP (Life Technologies, Inc.) wurde als das chromogene Substrat verwendet.
- Aminoterminale Sequenzanalyse. Proteine wurden einer Polyacrylamid-Gelelektrophorese in Anwesenheit von SDS unter Verwendung des Puffersystems von Laemmli (Laemmli, U. K. et al. (1970) Nature 227: 680–685) unterworfen. Proteine wurden elektrophoretisch von dem Gel auf eine Problot-Membran (Applied Biosystems, Foster City, CA) gemäß den Anweisungen des Herstellers transferiert. Proteine wurden durch Coomassie-Blau-Färbung sichtbar gemacht und die 63 kDa und 55 kDa HEV-ORF2-Proteine wurden für eine aminoterminale Sequenzanalyse unter Verwendung eines Applied Biosystems Modell 473 Gas/gepulste flüssige Phase-Proteinsequenzierer mit on-line-PTH-Analysierer ausgeschnitten.
- Analyse interner Aminosäuresequenz. Proteine wurden wie vorstehend beschrieben einer Elektrophorese unterworfen. Proteine wurden auf Nitrocellulosemembranen transferiert und mit Ponceau S-Färbung sichtbar gemacht. Die relevanten Banden wurden aus der Membran geschnitten und für einen proteolytischen in situ-Verdau mit Lys C (Boehringer Mannheim, Indianapolis, IN) gemäß dem Verfahren von Abersold et al. prozessiert (Abersold, R. H. et al. (1987) Proc. Natl. Acad. Sci. USA 84: 6970–6974). Die Lys C-abgeleiteten Fragmente wurden unter Verwendung eines Hochdruck-Flüssigchromatographiesystems von Waters Associates (Medford, MA) und einer reverse Phase-Säule, Vydac C4 (Hesperia, CA), isoliert. Die Aminosäuresequenzen der isolierten Peptide wurden unter Verwendung eines Proteinsequenzie rers, Modell 477A, und on-line-PTH-Analysierers, Modell 120A, von Applied Biosystems bestimmt.
- Aminosäureanalyse. Die Aminosäurezusammensetzungen der vorstehend beschriebenen Lys C-abgeleiteten Fragmente wurden nach einer Dampfphasen-Hydrolyse in 6 N HCl bei 150°C für eine Stunde unter Verwendung einer Waters Pico Tag Workstation bestimmt. Aminosäuren wurden mit Phenylisothiocyanat (PTC) derivatisiert und die erhaltenen PTC-Aminosäuren wurden unter Verwendung eines Waters Pico Tag Aminosäureanalysesystems getrennt und quantifiziert.
- Carboxyterminale Sequenzanalyse. Immobilisierte Carboxypeptidase Y (Pierce, Rockford, IL) wurde für die sequenzielle Freisetzung von Aminosäuren vom Carboxyterminus des 55 kDa-HEV-Proteins verwendet. Ungefähr 150 µg des Proteins in 800 µl 0,05 M Natriumacetatpuffer pH 5,5 wurden mit einer 200 µl-Suspension des Harzes bei 37°C gemischt. Aliquots des Überstands (100 µl) wurden bei 0, 5, 15, 30, 60, 90 und 120 Minuten entnommen. Ein abschließendes Aliquot wurde bei 16 Stunden gesammelt. Die Proben wurden unter vermindertem Druck getrocknet und eine Aminosäureanalyse wie vorstehend beschrieben ohne den Hydrolyseschritt unterworfen.
- Massenspektroskopie. Massenspektrometrischer Nachweis von gereinigten Proteinen wurde mit einem Dreistufen-Quadrupol-Massenspektrometer, Perkin-Elmer, Sciex API-III (Foster City, CA), das mit einer aufgesattelten Atmosphärendruck-Ionensprayquelle ausgestattet war, durchgeführt. Hochreiner Stickstoff diente sowohl als das Zerstäubergas (operativer Druck = 0,5 MPa) als auch als das Curtain-Gas (Flussrate = 0,8 1/Minute). Argon wurde als das Zielgas mit einer Kollisionsgasmasse von 3 × 1015 Atomen/cm2 verwendet. Der Scanbereich der Massenspektren von mIz 100–1500 positiven Ionen wurde durch direkte Infusion von 50 µl/Minute von Rinderserumalbumin-Standardlösungen, die 1:200 verdünnt waren, in die mobile Phase mit einer Spritzenpumpe, Harvard Apparatus Modell 11 (Southnatick, MA), erreicht. Spektren wurden bei 1,0 Sekundenintervallen aufgenommen. Kapillarspannung wurde bei 2 kV und 60°C aufrecht erhalten.
- Die zeitliche Expression von HEV-ORF2-Genprodukten wurde zur Identifizierung prozessierter rekombinanter HEV-Proteine untersucht. Sf-9-Insektenzellen, die als Suspensionskulturen in serumfreiem Medium kultiviert wurden, wurden mit rekombinanten Baculoviren, die das Volllängen-Hepatitis E-Virus-Capsidgen (Pakista ni-Stamm) (
11 ) kodieren, infiziert. Zell-Lysate und Medienüberstände wurden von den Virusinfektionen täglich für vier aufeinander folgende Tage geerntet. Ergebnisse von SDS-PAGE- und Western Blot-Analysen von HEV-Zell-Lysaten zeigten die Anwesenheit eines HEV-ORF2-72 kDa-Proteins einen Tag nach Infektion (p.i.), das danach verschwand (12 ). Zwei Tage p.i. waren 63 und 55 kDa HEV-Proteine in infizierten Zellen vorhanden. Das 55 kDa-HEV-Protein wurde in infizierten Zellen drei Tage p.i. vorherrschend (12 ). Das reichlich vorhandene Protein bei 63–65 kDa, das von zwei bis vier Tagen nach Infektion beobachtet wurde, wurde als die Baculovirus-Chitinase und nicht das HEV-63 kDA-Protein identifiziert. Ein 53 kDa HEV-Protein wurde in Medienüberständen von infizierten Zellen einen Tag p.i. sekretiert und war drei Tage p.i. maximal vorhanden. Diese Ergebnisse zeigten, dass eine stochastische proteolytische Spaltung des primären 72 kDa-HEV-Proteins auftrat, um ein endgültiges 55 kDa (Zell-Lysat) oder 53 kDa (Medien) HEV-Proteinprodukt zu erstellen. - HEV-Proteinreinigung. Die rekombinanten HEV 63 und 55 kDa-Proteine wurden durch Anionenaustauschchromatographie und Gelfiltration von Zell-Lysaten gereinigt, die durch NP-40-Lyse von Sf-9-Zellen, die mit rekombinantem bHEV-ORF2-fl-Virus oder verkürzten Viren infiziert und vier Tage p.i. geerntet worden waren, hergestellt wurden. Das sekretierte 53 kDa-Protein wurde von Medienüberständen von geernteten Virusinfektionen, die durch Zentrifugation geklärt worden waren, gereinigt und zehnfach durch Tangentialfluss-Ultrafiltration konzentriert. Zell-Lysate und konzentrierte Medienüberstände wurden mit Q-Beladungspuffer (50 mM Tris-HCl, pH 8,0, 10 mM NaCl) von Zellen, die mit dem 5'-doppelt traventierten Konstrukt infiziert worden waren, zehnfach verdünnt bzw. diafiltriert. Äquilibrierte Zell-Lysate (55 kDa-Protein) und Medienüberstände (53 kDa-Protein) wurden getrennt voneinander auf eine Q-Sepharose Fast Flow starker Anionenaustauscher-Säule geladen. HEV-55 kDa-Proteine wurden gebunden und bei einer Innenstärke von 140 mM NaCl eluiert (
13A ). HEV-Proteinfraktionen von chromatographisch getrennten Zell-Lysaten und Überständen wurden vereinigt, mittels Passage durch eine Sephacryl-Gel-25-Säule entsalzt und einer zweiten Runde an Anionenaustauscherchromatographie unter Verwendung einer SOURCE 15 Q starke Anionen-Hochdurchsatz-Säule unterworfen. HEV-Proteine wurden gebunden und dann bei 140 mM NaCl eluiert (13B ). HEV-Protein-Peak-Fraktionen wurden zusammengeführt und durch Gelfiltration unter Verwendung einer Sephacryl-S-200-Säule fraktioniert (13C ). SDS-PAGE- und Western Blot-Analysen der 55 kDa-Proteinfraktionen zeigten, dass das 55 kDa-Protein von HEV-Ursprung war (14 , unteres Schaubild). Von Coomassie-Blau-gefärbten Proteingelen wurde die Reinheit des 55 kDa-Proteins auf 99% oder größer geschätzt (14 , oberes Schaubild). - Aminoterminale Sequenzanalyse. Zur Bestimmung der Aminotermini der rekombinanten HEV-63- und 55 kDa-Proteine, die während bHEV-Infektion von Insektenzellen nachgewiesen wurden, wurde eine aminoterminale Aminosäuresequenzanalyse durchgeführt. Zusammengeführte HEV-Proteinfraktionen wurden von Q-Sepharose Fast Flow-Säulen gesammelt, die mit verdünnten Zell-Lysaten von Sf-9-Insektenzellen, die mit bHEV-ORF2-fl-Virus infiziert und zwei Tage p.i. geerntet worden waren, beladen wurden. Zwei HEV-Proteine wurden von den Peak-Q-Fraktionen bei 140 mM NaCl bei einem Verhältnis von 1:20 (63 kDa:55 kDa) gereinigt. Direkter Edman-Abbau der HEV 63 kDa- und 55 kDa-Proteinbanden, die von der ProBlot-Membran ausgeschnitten wurden, führte zu einer identischen Aminosäuresequenz über 20 Zyklen (Tabelle 9). Tabelle 9. Aminoterminale Aminosäuresequenzanalyse von rekombinanten HEV 63 (SEQ ID NO: 110) und 55 (SEQ ID NO: 111) kDa-Proteinen, die von Zell-Lysaten gereinigt wurden.
Zyklus des Aminosäureanalysators HEV 55 kD HEV 63 kD 1 A A 2 A A 3 P P 4 L L 5 T T 6 A A 7 V V 8 A A 9 P P 10 A A 11 H H 12 D D 13 T T 14 P P 15 P P 16 V V 17 P P 18 D D 19 V V 20 D D - Die Sequenz entsprach Resten 112 bis 131 des offenen Leserahmens 2 des HEV-Genoms. Diese Ergebnisse zeigten, dass der Unterschied in dem scheinbaren Mole kulargewicht zwischen den zwei immunoreaktiven Proteinen in carboxyterminalen Verkürzungen begründet war.
- Analyse interner Aminosäuresequenzen. Um die geteilte Identität der rekombinanten HEV 63 und 55 kDa-Proteine weiter zu bestimmen, wurden ein Peptidaseverdau und eine Fraktionierung durchgeführt. Gereinigtes 55 kDa HEV-Protein wurde mit Lys C-Protease verdaut, da die Spezifität dieses Enzyms für eine Spaltung carboxyterminal zu Lysinresten geeigneter als Trypsin für eine Peptidproduktion und Aminosäuresequenzbestimmung vom 55 kDa HEV-Protein erschien. Das Peptidprofil des erhaltenen Lys C-Verdaus ist in
15 gezeigt. - Aliquots der Peaks wurden einer Aminosäuresequenzanalyse unterworfen. Aminosäuresequenzen von internen Peptiden des rekombinanten HEV ORF2 55 kDa-Proteins entsprachen der erwarteten Aminosäuresequenz des HEV ORF2 (Pakistani-Stamm). Peptide, die Aminosäuresequenzen von dem Aminosäurebereich 607 bis 670 von HEV-ORF2 enthielten, wurden nicht gefunden. Von besonderem Interesse war Fraktion 24, die 52 Zyklen einer klaren Sequenz lieferte, die Aminosäureresten 554 bis 606 von HEV-ORF-2 entsprach. Erhöhungen in PTH-Leucin bei Zyklen 53 oder 55 (Reste 606 oder 608) wurden nicht beobachtet, obwohl eine Erhöhung im PTH-Alanin in Zyklus 54 beobachtet wurde. Da > 50 Aminosäurereste einer lesbaren Aminosäuresequenz in unserem Labor nicht alltäglich waren, war nicht klar, ob das Scheitern, zusätzliche Sequenzdaten zu erhalten, durch ein Fehlen eines Signals durch Erreichen des Endes des Peptids (d. h. der Carboxyterminus des Proteins) oder durch ein Scheitern der Edman-Chemie bedingt war. Daher war eine Bestimmung des Carboxyterminus des rekombinanten HEV-ORF2-55 kDa-Proteins durch mehrere andere Mittel notwendig.
- Analyse der Aminosäurezusammensetzung: Ein alternatives Mittel zur Bestimmung, ob Aminosäuren 606 bis 608 des rekombinanten HEV-ORF2-55 kDa-Proteins in Fraktion 24 des Lys C-Verdaus vorhanden waren, war eine Analyse der Aminosäurezusammensetzung dieses Peptids. Die Ergebnisse der Aminosäureanalyse eines Aliquots von Fraktion 24 ist in Tabelle 10 gezeigt. Tabelle 10. Zusammenfassung der Analyse der Aminosäurezusammensetzung von Fraktion 24 von Lys-C-verdautem HEV 55 kDa-Protein.
Aminosäure Erwartet Beobachtet Asn + Asp 4 4.4 Gln + Glu 2 3.2 Ser 6 5.7 Gly 4 6.3 His 2 2.1 Arg 1 2.0 Thr 5 5.0 Ala 10 10 Pro 3 3.3 Tyr 4 3.5 Val 6 6.1 Met 0 .7 Cys* 0 0* Ile 2 2.7 Leu 6 6.3 Phe 0 .6 Lys 0 .9 Normalisiert auf 10 Ala Keine Derivatisierung von Cys wurde vor Hydrolyse durchgeführt - Diese Analyse zeigte, das das Scheitern, Aminosäuresequenzdaten nach Zyklus 54 (Rest 607) zu erhalten, durch die Tatsache begründet war, dass die Aminosäuresequenzierung den Carboxyterminus des 55 kDa-Proteins erreicht hatte. Die Ergebnisse stimmten mit dem bei Leucin 607 endenden Peptid überein. Obwohl diese Analyse andere geringe Variationen enthielt, zeigte sie deutlich, dass das Peptid weit nach einem früheren Lysinrest (Rest 600) im HEV-ORF-2 endete.
- Carboxyterminale Sequenzanalyse. Ein weiteres Mittel zur Bestimmung des Carboxyterminus des rekombinanten HEV-ORF2-55 kDa-Proteins war eine carboxyterminale Aminosäureanalyse von Carboxypeptidase-verdautem 55 kDa-Protein. Aminosäureanalyse der freien Aminosäuren, die während einer zeitlich festgelegten Inkubation mit immobilisierter Carboxypeptidase Y freigesetzt wurden, zeigte eine schnelle Erhöhung an Leucin gefolgt von Valin, Serin und Histidin (
16 ). - Keine deutlichen Erhöhungen der Mengen anderer Aminosäuren wurden beobachtet. Diese Ergebnisse untermauern ein Festlegen des Carboxyterminus des rekombinanten HEV-ORF2-55 kDa-Proteins bei Aminosäure Leucin 607.
- Massenspektrometrische Analyse. Das erwartete Molekulargewicht des HEV-55 kDa-Proteins (Aminosäuren 112–607 von HEV-ORF2) von der Nukleotidsequenz von HEV-ORF2 (Pakistani-Stamm) wurde auf 53 kDa geschätzt. Um eine absolute Masse dieses Proteins zu erhalten, wurde eine Elektronenspray-Massenspektroskopie des gereinigten rekombinanten HEV-55 kDa-Proteins durchgeführt. Das Ergebnis von mehreren Runden an MS-Messungen war, dass ein einzelnes Polypeptid mit einer Molekularmasse von ~56000 Dalton in der gereinigten Proteinpräparation vorhanden war (
17 ). Da Massenspektroskopie einen Genauigkeitsgrad von 0,01% hat, wurde die Schlussfolgerung untermauert, dass das HEV-55 kDa-Protein durch sowohl N- als auch C-terminale proteolytische Spaltungen erstellt wurde. - Kinetik der Expression von verkürztem HEV-ORF2-Protein in Insektenzellen. Zur Bestimmung, ob primäre Proteine, die an den Amino- und/oder Carboxytermini des HEV-ORF2 deletiert waren, stabil und mit hohen Niveaus in Insektenzellen exprimiert werden konnten, wurden 5' und 5'-3' verkürzte Deletionsmutanten des HEV-ORF2 in Baculovirusvektoren kloniert. Die Ergebnisse von Infektionen mit bHEV-ORF2 5' tr- und bHEV-ORF2 5'-3' tr-Viren zeigten, dass die 63 und 55 kDa-Proteine beide in Insektenzellen exprimiert wurden (
18 ). Jedoch war das 55 kDa-Protein drei Tage p.i. in der bHEV-ORF2-5' tr-Infektion > 50-fach mehr vorhanden und war in bHEV-ORF2-5'-3' tr-Virusinfektionen ausschließlich vorhanden. Ein 53 kDa-Protein wurde auch innerhalb des ersten Tages der Infektion mit beiden Viren in Überstandsmedien sekretiert und erreichte drei Tage p.i. maximale Niveaus. Die Menge an sekretiertem 53 kDa-Protein war von Insektenzellen, die mit dem bHEV-ORF2 5'-3' tr-Virus infiziert worden waren, mehr als 20-fach mehr vorhanden als von Zellen, die mit dem bHEV-ORF2 5' tr-Virus infiziert worden waren. Das 55 kDa-Protein wurde von Zell-Lysaten von beiden viralen Infektionen gereinigt und das 53 kDa-Protein wurde vom Überstandsmedium durch die vorstehend beschriebenen Reinigungsschemata gereinigt. Die Amino- und Carboxytermini des sekretierten 53 kDa-Proteins sind als Aminosäuren 112 und 578 von HEV-ORF2 identifiziert worden und es ist im ELISA gezeigt worden, dass das 53 kDa-Protein antigenisch ist. Das erwartete Molekulargewicht des 53 kDa-Proteins war 50 kDa, aber es wurde durch Massenspektroskopie gezeigt, dass das Protein eine molekulare Masse von ungefähr 53 kDa hat. - Ortsgerichtete PCR-Mutagenese des 112–607 bHEV wurde auch unter Verwendung eines Oligonukleotid-Primers, der das AUU-Codon und umgebende Nukleotide bei Aminosäure 578 (Pakistani-Stamm HEV-ORF2), zur Erstellung einer Substitution von Arginin durch Isoleucin bei Aminosäure 578 durchgeführt. Andere Mutanten des 112–607 bHEV umfassten diejenigen mit Aminosäuresubstitution von Arginin durch Glycin, Serin oder Glutaminsäure bei Aminosäure 578. Diese Mutanten wurden wie vorstehend beschrieben unter Verwendung von Oligonukleotid-Primern, die Codons für die erwünschten Aminosäureänderungen enthielten, erstellt, Es wird angenommen, dass diese 112–607 bHEV-Mutanten das Gleichgewicht der Produktion von HEV-ORF2-Proteinen hin zu einem einzelnen Protein verschieben werden.
- BEISPIEL 18
- Vakzinstudien in Rhesusaffen
- Primaten. 32 Rhesusaffen (Macacca mulatta), die in einem sensitiven ELISA negativ (< 1,10) für HEV-Antikörper (Anti-HEV) waren (Tsarev SA, et al. J. Infect. Dis. (1993), 89: 369–78), wurden in dieser Studie verwendet.
- HEV-Belastungsstammlösung. Der Pakistani-HEV-Stamm SAR-55 [Igbal M., et al. J. Trop. Med. Hyg. 1989, 40, 438–443] (menschliche Fäkalien) oder der mexikanische HEV-Stamm Mex-14 [Velazquez O., et al. JAMA (1990), 263: 3281–5] (Affenfäkalien, bereitgestellt durch das CDC) wurde als eine Quelle für Belastungs-Virus verwendet. Eine Suspension [in seronegativem Cynomolgus (Macacca fascicularis)-Serum] an Fäkalien, die den Pakistani- oder den mexikanischen HEV-Stamm enthielt und so verdünnt war, dass sie 10000 infektiöse Dosen für Affen (MID50) enthielt, wurde zur intravenösen Inokulation von Tieren verwendet.
- Inokula für Immunisierung. 55 kDa-ORF-2-Protein [Tsarev SA, et al. Prospects for prevention of hepatitis E. In: Enterically transmitted hepatitis viruses. (Y. Buisson, P. Coursaget, M. Kane, Hrsg.). La Simarre, Joueles-Tours, Frankreich (1996) S. 373–383], das von infizierten Insektenzellen (infiziert mit rekombinantem Baculovirus, der den kompletten ORF2 enthielt) gereinigt wurde, wurde mit Alaun wie beschrieben ausgefällt [Tsarev S. A. et al. Proc. Natl. Acad. Sci. USA, (1994), 191: 10198–202]. Die Wirksamkeit der Ausfällung war größer als 99% wie durch ELISA-Analyse des restlichen löslichen Antigens bestimmt wurde. Der Protein-Alaun-Komplex wurde bei +4°C bis zu ein Jahr gelagert.
- Inokulationsplan.
- Rhesusaffen wurden durch intramuskuläre Injektion von 0,5 ml Vakzin, das 50 µg, 10 µg, 2 µg oder 0,4 µg des Alaun-ausgefällten 55 kDa-Proteins enthielt, vakziniert. Zwei Dosen wurden in einem Abstand von einem Monat verabreicht. Anderen Tieren wurde 0,5 ml Alaun-Suspension ohne das rekombinante Protein (Placebo) injiziert.
- Beobachtung von Primaten. Perkutane Nadelbiopsien der Leber und Proben von Serum und Fäkalien wurden vor Inokulation und wöchentlich für 15 Wochen nach Inokulation gesammelt. Seren wurden auf Niveaus von Alanin-Aminotransferase (ALT) mit kommerziell erhältlichen Tests (Metpath Inc., Rockville, MD) untersucht. Biochemische Anzeichen für Hepatitis wurden als eine zweifache oder größere Erhöhung des nach Inokulation/vor Inokulation-Verhältnisses von ALT definiert. Leberbiopsie wurde durchgeführt und Histopathologie wurde bewertet wie beschrieben [Tsarev S. A. et al. Proc. Natl. Acad. Sci. USA (1994), 191: 10198–202]. Klinische Auswertung der Tiere wurde blind durchgeführt. Der Anti-HEV-ELISA und reverse Transkriptase-Polymerasekettenreaktion (RT-PCR) wurden wie beschrieben durchgeführt [Tsarev S. A. et al. Proc. Natl. Acad. Sci. USA, 1994, 191: 10198–202]. Zur Quantifizierung wurden PCR-positive aufeinander folgende Seren oder Fäkalien von jedem Tier zusammengeführt und seriell in 10-fachen Abstufungen in Kälberserum verdünnt. 100 µl jeder Verdünnung wurden für eine RNA-Extraktion und RT-PCR verwendet. Das PCR-Protokoll, das in dieser Studie verwendet wurde, konnte so wenig wie 10 MID50 an HEV pro ml Serum und so wenig wie 100 MID50 pro Gramm Fäkalien nachweisen.
- Statistische Analyse. Student-t-Tests wurden für einen paarweisen Vergleich von quantitativen Parametern von Hepatitis und HEV-Infektion einer Placebo-Gruppe gegen die Vakzinierungsgruppe nach Belastung und einer Placebo-Gruppe gegen die Gruppe, die mit dem heterologen Virus belastet worden war, verwendet. Der Dunnett-Test wurde für einen multiplen Vergleich der Placebo-Gruppe gegen Gruppen, die mit unterschiedlichen Dosen des rekombinanten Vakzins vakziniert worden waren, verwendet. Der Tukley-Test wurde für multiple Vergleiche von Anti-HEV-Titern zum Zeitpunkt der Belastung in Tieren, die mit unterschiedlichen Dosen vakziniert worden waren, verwendet.
- Für eine statistische Analyse wurden Serumproben, die < 10 HEV-Genome in 1 ml Serum enthielten, ein Titer von 1:1 zugewiesen und fäkalen Proben, die < 100 HEV-Genome in 1 g Fäkalien enthielten, wurde ein Titer von 1:10 zugewiesen.
- ERGEBNISSE
- Hepatitis E-Infektion in den Placebo-Gruppen. Jeder der vier Rhesusaffen, die mit nur Alaun vakziniert und mit dem HEV-Stamm SAR-55 belastet worden waren, entwickelte Hepatitis: nach/vor-Peak-ALT-Verhältnisse in diesen Tieren waren deutlich höher als der Cut-off-Wert von 2,0 und reichten von 3,1 bis 10,6 (Tabelle 12).
- Hepatitis wurde durch die Ergebnisse der histologischen Tests bestätigt. Der kumulative histopathologische Wert reichte von 4,5+ bis 6,0+. Virämie und Virusausscheidung wurden in jedem Tier überwacht. Virämie trat für 5 bis 6 Wochen auf und Virus wurde insgesamt 5 bis 7 Wochen ausgeschieden. Positive Serum- oder fäkale Proben wurden vereinigt und HEV-Genomtiter wurden in diesen Vereinigungen für jedes Tier bestimmt. Der HEV-Genomtiter reichte von 103 bis 104 in vereinigten Seren und von 106 bis 108 in vereinigten fäkalen Proben. Die HEV-Genomtiter waren zu denjenigen vergleichbar, die wir vorher für Cynomolgus-Affen, die mit dem gleichen SAR-55-Stamm von HEV belastet worden waren, berichteten (Tsarev S. A. et al. Proc. Natl. Acad. Sci. USA, (1994), 191: 10198–202). Dauer der Virämie und Virusausscheidung waren auch vergleichbar.
- Jedes der vier Tiere, die mit dem Mex-14-Stamm von HEV belastet worden waren, entwickelte Hepatitis mit quantitativen Parametern der Krankheit, was histopathologische Werte erwarten ließ, die ähnlich zu denjenigen von Tieren sind, die mit dem SAR-55-Stamm belastet worden waren (Tabelle 13).
- Quantitative Parameter der Infektion waren auch in den zwei Gruppen an Tieren ähnlich. Daher waren die HEV-Belastungsstammlösungen fähig, Hepatitis in jedem und allen belasteten Tieren auszulösen, und konnten daher für eine Validierung der Vakzinwirksamkeit gegen Hepatitis E verwendet werden.
- Hepatitis E-Infektion in der Gruppe, die nach Aussetzung vakziniert wurde. Vier Tiere wurden mit dem SAR-55-Stamm belastet. 48 Stunden nach Belastung wurden diese Tiere mit einer 50 µg-Dosis Vakzin gefolgt von einer Auffrischdosis (50 µg) einen Monat später vakziniert. Deutliche Unterschiede in Parametern der Krankheit oder der Infektion wurden in dieser Gruppe verglichen mit der Placebo-Gruppe nicht gefunden, mit der Ausnahme, dass die Dauer der Virämie und viralen Ausscheidung 1,5-fach bzw. 1,7-fach verringert war (Daten nicht gezeigt).
- Vakzinierung. Alle mit der 50 µg, 10 µg oder 2 µg Vakzindosis vakzinierten Primaten und 3 von 4 mit der 0,4 µg-Dosis des rekombinanten Proteins vakzinierten Primaten serokonvertierten zu HEV nach der ersten Immunisierung (Tabellen 12 und 13). Eine direkte Korrelation zwischen Vakzindosis und Anti-HEV-Titer wurde nach der ersten Dosis beobachtet; ein geometrisches Mittel (GM) von 1:32 für die 0,4 µg-Dosis, 1:316 für die 2 µg-Dosis, 1:1000 für die 10 µg-Dosis und 1:3200 für die 50 µg-Dosis. Wenn die zweite Vakzindosis verabreicht wurde, wurden Dosis-bezogene Unterschiede in GM-Titern noch einen Monat nach der zweiten Vakzinierung beobachtet, aber der Bereich war enger (zwischen 1:1800 und 1:5600 wie in Tabelle 14 zu sehen).
- Statistische Analyse unter Verwendung eines multiplen Vergleichstests für Anti-HEV-GM-Titer zeigte, dass die Dosis-bezogenen Unterschiede in GM-Titern nach zwei Vakzindosen nicht signifikant waren. Zu diesem Zeitpunkt wurden die Rhesusaffen belastet.
- Homologe Belastungen. Alle 16 Tiere, die mit einer jeglichen der vier Vakzindosen vakziniert wurden, waren gemäß dem biochemischen Kriterium gegen Hepatitis geschützt, da keines erhöhte Serum-ALT-Niveaus entwickelte (Tabelle 12). Histologische Änderungen wurden nur in zwei der 16 Tiere gefunden und diese hatten die zwei geringsten Vakzindosen erhalten. Die histologischen Abweichungen waren minimal und könnten in einem dieser zwei Tiere (Rhesus-5978) nicht mal mit einer HEV-Infektion zusammenhängen, da ähnliche Abweichungen auch in Vorinokulationsleberproben gefunden wurden. Insgesamt waren alle vier Tiergruppen, die zweimal mit 50 µg, 10 µg, 2 µg oder 0,4 µg Vakzindosen vakziniert worden waren, gegen Hepatitis geschützt und quantitative Parameter von Hepatitis E waren in jeder dieser vier Gruppen von denjenigen in der Placebo-Gruppe statistisch unterschiedlich (Tabelle 14).
- Obwohl Tiere in allen vakzinierten Gruppen gegen Hepatitis E-Krankheit geschützt waren, waren sie nicht gegen eine Infektion mit HEV geschützt. Obwohl Virustiter in vakzinierten Tieren statistisch geringer als diejenigen in den Placebo-Gruppen waren, waren die Dauer der Virämie und viralen Ausscheidung in der Mehrheit der Fälle nicht signifikant verringert. Verglichen zu der Placebo-Gruppe war das Niveau an Virämie in den vakzinierten Tieren etwa 80-fach verringert und das Niveau an viraler Ausscheidung war im Durchschnitt etwa 1000-fach verringert. Zwei Tiere waren gegen Virämie mit dem Mex-14 HEV-Stamm, der sich kinetisch und geographisch am meisten von dem Vakzinstamm unterschied, geschützt und waren gegen Hepatitis durch Verabreichung von zwei 50 µg-Dosen an rekombinantem Vakzin geschützt (Tabelle 13). Histologische oder biochemische Anzeichen für Hepatitis wurde in keinem dieser Tiere nachgewiesen. Wenn immunisierte Tiere als Gruppe mit der Placebo-Gruppe verglichen wurden, waren die Unterschiede in der Äußerung der Krankheit statistisch signifikant (Tabelle 14). Jedoch waren wie im Fall von homologer Belastung die meisten Tiere nicht gegen eine Infektion mit HEV geschützt. Sowohl Virämie als auch virale Ausscheidung wurden in drei Tieren nachgewiesen. Das vierte Tier zeigte keins von beidem und war daher komplett gegen Infektion geschützt. Niveaus an Virämie und viraler Ausscheidung waren deutlich verringert (etwa 180-fach und 1800-fach), wenn sie mit Tieren verglichen wurden, die mit dem Placebo vakziniert worden waren. Der Unterschied in der Dauer an viraler Ausscheidung war signifikant, aber der einer Virämie war es nicht.
- Zusammengefasst zeigten diese Experimente, dass eine Dosis des rekombinanten Proteins so gering wie 0,4 µg, die zweifach verabreicht wurde, Rhesusaffen vor Hepatitis schützte. Signifikante Unterschiede in Anti-HEV-GM-Titern nach zwei Vakzindosen, die von 0,4 µg bis 50 µg reichten, wurden nicht beobachtet. Wenn sie mit dem homologen Virusstamm belastet wurden, waren alle vakzinierten Tiere gegen Hepatitis E wie durch ALT-Erhöhungen geschützt und nur zwei Tiere, die beide die geringste Vakzindosis erhielten, zeigten eine minimale Histopathologie. Die schützende Wirkung des Vakzins wurde durch Multi-Gruppenvergleich quantifiziert, was anzeigte, dass mit der Ausnahme der Gruppe, die nach Belastung vakziniert worden war, quantitative Parameter von Hepatitis in allen vakzinierten Primaten geringer als diejenigen in der Placebo-Gruppe waren, und dieser Unterschied war statistisch signifikant. Zusätzlich waren vakzinierte Tiere, die die 50 µg-Dosis des Vakzins, die einzige getestete Dosis, zweimal erhielten, vor heterologer Belastung mit dem genetisch und geographisch am weitesten entfernten HEV-Stamm, der bis heute identifiziert wurde, geschützt. Im Gegensatz dazu war eine Vakzinierung nach Belastung nicht erfolgreich. Alle Tiere, die 48 Stunden nach Belastung vakziniert worden waren, entwickelten gemäß sowohl biochemischen als auch histologischen Kriterien Hepatitis.
- Obwohl seropositive Primaten gegen Hepatitis E nach Belastung mit einer hohen Dosis an HEV geschützt waren, waren die meisten davon nicht gegen eine HEV-Infektion geschützt. Dies ist möglicherweise nicht überraschend, da dieser Virus, der normalerweise über den oralen Weg übertragen wird, zur Absicherung einer gleichförmigen Aussetzung intravenös verabreicht wurde. Jedoch war das Ausmaß einer Infektion wie durch Niveaus an Virämie und viraler Ausscheidung gemessen in allen vakzinierten Tieren verglichen zu Placebo-Tieren deutlich verringert und tatsächlich war ein Tier, das mit dem heterologen Stamm belastet worden war, komplett gegen Infektion mit HEV geschützt und zwei Tiere, die mit dem homologen HEV-Stamm belastet worden waren, schieden Virus aus, hatten aber keine nachweisbare Virämie. Der höhere Prozentsatz an Tieren, die komplett gegen Infektion in einer vorhergehenden Studie geschützt waren [Tsarev S. A. et al. Proc. Natl. Acad. Sci. USA, (1994), 191: 10198–202], könnte durch die Tatsache erklärt werden, dass wir in der vorhergehenden Studie sowohl 1000 als auch 10000 MID50-Dosen an Belastungsvirus verwendeten, während wir in dieser Studie nur die höhere Dosis verwendet haben. Da es eine Dosis-abhängige Antwort auf HEV-Infektion in Primaten gibt [Tsarev SA, et al. Prospects for prevention of hepatitis E. In: Enterically transmitted hepatitis viruses. (Y. Buisson, P. Coursaget, M. Kane, Hrsg.). La Simarre, Joueles-Tours, Frankreich, 1996, S. 373–383], wurde die höhere Dosis ausgewählt, um abzusichern, dass jedes nicht vakzinierte Tier eine ausgeprägte Hepatitis entwickelte.
- In dieser und der vorhergehenden Studie ist gezeigt worden, dass in allen Placebo- und vakzinierten Primaten der virale Titer im Serum ohne Ausnahme geringer war als der in Fäkalien (im Durchschnitt etwa 1000-fach). Dieses Ergebnis stimmt mit der Tatsache überein, dass HEV durch den fäkal-oralen Weg übertragen wird. In jedem vakzinierten Tier wurden verringerte Niveaus an Virämie und viraler Ausscheidung beobachtet, wenn sie mit Placebo-Tieren verglichen wurden. Jedoch war die Dauer an Virämie, obwohl sie in allen vakzinierten Primaten kürzer war, verglichen mit der in den Placebos in den meisten Fällen nicht signifikant verringert. In den einigen Dutzend untersuchten Primaten trat Virämie immer zusammen mit HEV-Ausscheidung in Fäkalien auf. Daher könnten Serumproben als der primäre Indikator einer viralen Infektion verwendet werden, wobei der Titer den Grad einer HEV-Infektion widerspiegelt. Dies ist eine wichtige Beobachtung, da Serumproben normalerweise leichter erhältlich sind als fäkale Proben.
- BEISPIEL 19
- Alternatives Reinigungsprotokoll für HEV-ORF2-Proteinprodukte.
- Das folgende Reinigungsprotokoll ist eine alternative Ausführungsform zu dem Reinigungsprotokoll, das auf Seiten 83–84 dieser Anmeldung offenbart ist.
- Das Reinigungsprotokoll ist wie folgt:
Rekombinante HEV-ORF2-Proteine wurden aus geklärten Lysaten und Überstandsmedien von Baculovirus-infizierten Zellen getrennt voneinander gereinigt. Das Zell-Rohlysat wurde 1:10 mit Beladungspuffer (50 mM Tris-HCl, pH 8,0, 10 mM NaCl) verdünnt. - Geklärte Überstände von infizierten Zellen wurden 10-fach durch Tangentialfluss-Ultrafiltration unter Verwendung einer spiralgewundenen Cellulose-Ultrafiltrationskartusche (S1Y10; 1 Sq. Ft. Fläche; 10000 MW Cutoff; Amicon, Beverly, MA) auf ei nem Amicon Proflux M-12-Ultrafiltrationssystem bei einer Rezirkulationsrate von 4 1/Minute und einem Transmembrandruck von 20 PSI konzentriert. Der konzentrierte Überstand wurde gegen vier Volumen Beladungspuffer diafiltriert.
- Das Diafiltrat oder verdünnte Rohlysat (1,5 Bettvolumen) wurde auf eine Q-Sepharose Fast Flow starker Anionenaustauscher-Säule (XK50-Säule, 5,0 × 7,5 cm, 150 ml; Pharmacia, Piscataway, NJ) bei einer Flussrate von 10,0 ml/Minute geladen. Die Säule wurde zuerst mit 1,0 Bettvolumen Beladungspuffer bei einer Flussrate von 10,0 ml/Minute gefolgt von einem zweiten Waschschritt mit 1,0 Bettvolumen Beladungspuffer bei einer Flussrate von 20 ml/-Minute gewaschen. Die Proteine wurden mit 7,5 Bettvolumen eines kontinuierlichen linearen Gradienten an NaCl von 10–300 mM in dem gleichen Puffer bei einer Flussrate von 20 ml/Minute eluiert.
- 10 µl Aliquots von Q-Sepharose-Säule (Pharmacia, Piscataway, NJ)-Peak-Proteinfraktionen wurden einer SDS-PAGE-Analyse zur Identifizierung von HEV-ORF2 (+)-Proteinfraktionen unterworfen. Vereinigte (+)-Fraktionen wurden durch Gelfiltration unter Verwendung von Sephadex G-25 (Pharmacia) und Beladungspuffer entsalzt. Die Peak-Proteinfraktion wurde gesammelt und auf eine Source 15 Q High Performance (Pharmacia) starker Anionenaustauscher-Säule zum Trennen von HEV ORF2-Polypeptiden geladen. Die Säule wurde wie vorstehend für Q-Sepharose-Flüssigchromatographie beschrieben gewaschen und eluiert. Vereinigte HEV-ORF2-Protein (+)-Fraktionen wurden wie vorstehend identifiziert, vereinigt und einer abschließenden Gelfiltration auf einer Superdex 75-Säule (Pharmacia) unter Verwendung von Phosphat-gepufferter Kochsalzlösung (pH 6,8) für eine abschließende Proteinreinigung unterworfen. HEV-ORF2-Proteinfraktionen wurden durch SDS-PAGE- und Western Blot-Analysen identifiziert.
- Durch dieses Protokoll gereinigtes HEV-ORF2-Protein ist für eine Formulierung als ein HEV-Vakzin zur Verwendung in klinischen Studien der Phasen I und II geeignet.
Claims (31)
- DNA-Molekül mit einer Sequenz, die aus Nukleotiden besteht, die für ein Hepatitis E-Virus offenes Leseraster 2-Protein kodieren, wobei das Protein seinen Aminoterminus bei der Aminosäure 112 des offenen Leserasters 2 und seinen Carboxyterminus bei der Aminosäure 578 oder 607 des offenen Leserasters 2 hat.
- DNA-Molekül nach Anspruch 1 mit einer Sequenz, die aus Nukleotiden besteht, die für die Aminosäuren 112 bis 607 eines Hepatitis E-Virus offenes Leseraster 2-Proteins kodieren.
- DNA-Molekül nach Anspruch 1 mit einer Sequenz, die aus Nukleotiden besteht, die für die Aminosäuren 112 bis 578 eines Hepatitis E-Virus offenes Leseraster 2-Proteins kodieren.
- DNA-Molekül nach Anspruch 1, wobei das Molekül für ein Protein kodiert, das seinen Aminoterminus bei der Aminosäure 112 von SEQ ID NO: 2 und seinen Carboxyterminus bei der Aminosäure 578 oder 607 von SEQ ID NO: 2 hat.
- DNA-Molekül nach Anspruch 2, wobei das Molekül für die Aminosäuren 112 bis 607 von SEQ ID NO: 2 kodiert.
- DNA-Molekül nach Anspruch 3, wobei das Molekül für die Aminosäuren 112 bis 578 von SEQ ID NO: 2 kodiert.
- Rekombinanter Expressionsvektor, der ein DNA-Molekül gemäß den Ansprüchen 1, 2, 3, 4, 5 oder 6 umfasst.
- Wirtszelle, die einen Expressionsvektor gemäß Anspruch 7 enthält.
- Verfahren zur Herstellung eines rekombinanten Hepatitis E-Virus offenes Leseraster 2-Proteins, wobei das Verfahren umfasst: (a) Kultivieren einer Wirtszelle nach Anspruch 8 unter Bedingungen, die für eine Expression des Proteins geeignet sind, und (b) Gewinnen des exprimierten Proteins aus der Wirtszelle.
- Hepatitis E-Virus offenes Leseraster 2-Protein, das seinen Aminoterminus bei der Aminosäure 112 des offenen Leserasters 2 und seinen Carboxyterminus bei der Aminosäure 578 oder 607 des offenen Leserasters 2 hat.
- Hepatitis E-Virus offenes Leseraster 2-Protein nach Anspruch 10, das aus den Aminosäuren 112 bis 607 eines Hepatitis E-Virus offenes Leseraster 2-Proteins besteht.
- Hepatitis E-Virus offenes Leseraster 2-Protein nach Anspruch 10, das aus den Aminosäuren 112 bis 578 eines Hepatitis E-Virus offenes Leseraster 2-Proteins besteht.
- Hepatitis E-Virus-Protein nach Anspruch 10, wobei das Protein seinen Aminoterminus bei der Aminosäure 112 von SEQ ID NO: 2 und seinen Carboxyterminus bei der Aminosäure 578 oder 607 von SEQ ID NO: 2 hat.
- Hepatitis E-Virus-Protein nach Anspruch 11, wobei das Protein aus den Aminosäuren 112 bis 607 von SEQ ID NO: 2 besteht.
- Hepatitis E-Virus-Protein nach Anspruch 12, wobei das Protein aus den Aminosäuren 112 bis 578 von SEQ ID NO: 2 besteht.
- Pharmazeutische Zusammensetzung, die das Protein nach Anspruch 10, 11, 13 oder 14 und ein geeignetes Exzipienz, Verdünnungsmittel oder einen geeigneten Träger umfasst.
- Verwendung des Proteins nach Anspruch 10, 11, 13 oder 14 zur Herstellung eines Medikaments für eine Verwendung bei einer Vermeidung von Hepatitis E in einem Säuger.
- Vakzine für ein Immunisieren eines Säugers gegen eine Hepatitis E-Infektion, wobei die Vakzine ein Protein gemäß Anspruch 10, 11, 13 oder 14 in einem pharmazeutisch verträglichen Träger umfasst.
- Kit zur Vermeidung von Hepatitis E in einem Säuger, wobei der Kit ein Protein gemäß Anspruch 10, 11, 13 oder 14 umfasst.
- Verfahren zum Nachweis von Antikörpern gegen Hepatitis E-Virus in einer biologischen Probe, wobei das Verfahren umfasst: (a) Kontaktieren der Probe mit einem Hepatitis E-Virus offenes Leseraster 2-Protein, das seinen Aminoterminus bei der Aminosäure 112 des offenen Leserasters 2 und seinen Carboxyterminus bei der Aminosäure 578 oder 607 des offenen Leserasters 2 hat, und (b) Nachweis von Immunkomplexen, die zwischen dem Protein und den Antikörpern gebildet werden, wobei ein Nachweis der Komplexe das Vorhandensein von Antikörpern gegen Hepatitis E-Virus in der Probe anzeigt.
- Verfahren nach Anspruch 20, wobei das Hepatitis E-Virus offenes Leseraster 2-Protein aus den Aminosäuren 112 bis 607 eines Hepatitis E-Virus offenes Leseraster 2-Proteins besteht.
- Verfahren nach Anspruch 20, wobei das Hepatitis E-Virus offenes Leseraster 2-Protein aus den Aminosäuren 112 bis 578 eines Hepatitis E-Virus offenes Leseraster 2-Proteins besteht.
- Verfahren nach Anspruch 20, wobei das Protein seinen Aminoterminus bei der Aminosäure 112 von SEQ ID NO: 2 und seinen Carboxyterminus bei der Aminosäure 578 oder 607 von SEQ ID NO: 2 hat.
- Verfahren nach Anspruch 21, wobei das Protein aus den Aminosäuren 112 bis 607 von SEQ ID NO: 2 besteht.
- Verfahren nach Anspruch 22, wobei das Protein aus den Aminosäuren 112 bis 578 von SEQ ID NO: 2 besteht.
- Kit für eine Verwendung in einem Verfahren zum Nachweis von Antikörpern gegen Hepatitis E-Virus in einer biologischen Probe, wobei der Kit ein Hepatitis E-Virus offenes Leseraster 2-Protein umfasst, das seinen Aminoterminus bei der Aminosäure 112 des offenen Leserasters 2 und seinen Carboxyterminus bei der Aminosäure 578 oder 607 des offenen Leserasters 2 hat.
- Kit nach Anspruch 26, wobei der Kit ein Hepatitis E-Virus offenes Leseraster 2-Protein umfasst, das aus den Aminosäuren 112 bis 607 eines Hepatitis E-Virus offenes Leseraster 2-Proteins besteht.
- Kit nach Anspruch 26, wobei der Kit ein Hepatitis E-Virus offenes Leseraster 2-Protein umfasst, das aus den Aminosäuren 112 bis 578 eines Hepatitis E-Virus offenes Leseraster 2-Proteins besteht.
- Kit nach Anspruch 26, wobei das Protein seinen Aminoterminus bei der Aminosäure 112 von SEQ ID NO: 2 und seinen Carboxyterminus bei einer Aminosäure in dem Bereich der Aminosäuren 578 bis 607 von SEQ ID NO: 2 hat.
- Kit nach Anspruch 27, wobei das Protein aus den Aminosäuren 112 bis 607 von SEQ ID NO: 2 besteht.
- Kit nach Anspruch 28, wobei das Protein aus den Aminosäuren 112 bis 578 von SEQ ID NO: 2 besteht.
Applications Claiming Priority (3)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| US840316 | 1997-04-11 | ||
| US08/840,316 US6054567A (en) | 1997-04-11 | 1997-04-11 | Recombinant proteins of a pakistani strain of hepatitis E and their use in diagnostic methods and vaccines |
| PCT/US1998/007418 WO1998046761A1 (en) | 1997-04-11 | 1998-04-09 | Recombinant proteins of a pakistani strain of hepatitis e and their use in diagnostic methods and vaccines |
Publications (2)
| Publication Number | Publication Date |
|---|---|
| DE69839242D1 DE69839242D1 (de) | 2008-04-24 |
| DE69839242T2 true DE69839242T2 (de) | 2009-03-12 |
Family
ID=25282015
Family Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| DE69839242T Expired - Lifetime DE69839242T2 (de) | 1997-04-11 | 1998-04-09 | Rrekombinante proteine eines pakistani-stammes von hepatitis-e-virus, ihre verwendung in diagnotischen verfahren und als impfstoff |
Country Status (10)
| Country | Link |
|---|---|
| US (1) | US6054567A (de) |
| EP (2) | EP1958958B1 (de) |
| JP (1) | JP4390293B2 (de) |
| CN (1) | CN1202252C (de) |
| AT (2) | ATE389021T1 (de) |
| AU (1) | AU739915B2 (de) |
| CA (1) | CA2286399C (de) |
| DE (1) | DE69839242T2 (de) |
| ES (1) | ES2301195T3 (de) |
| WO (1) | WO1998046761A1 (de) |
Families Citing this family (6)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| CN101367869B (zh) * | 2000-09-30 | 2012-12-05 | 北京万泰生物药业股份有限公司 | 用于预防、诊断及治疗戊型肝炎病毒的多肽,及它们作为诊断试剂和疫苗 |
| US7005130B2 (en) * | 2001-01-05 | 2006-02-28 | Virginia Tech Intellectual Properties, Inc. | Avian hepatitis E virus, vaccines and methods of protecting against avian hepatitis-splenomegaly syndrome and mammalian hepatitis E |
| AU2002308593A1 (en) * | 2001-05-07 | 2002-11-18 | The Government Of The United States Of America, As Represented By The Secretary, Department Of Healt | Recombinant orf2 proteins of the swine hepatitis e virus and their use as a vaccine and as a diagnostic reagent for medical and veterinary applications |
| WO2003068788A1 (en) * | 2002-02-13 | 2003-08-21 | Medimolecular Pty. Ltd. | Method of isolating nucleic acids from stool samples |
| US20090305294A1 (en) * | 2003-02-13 | 2009-12-10 | Medimolecular Pty Ltd | Method of isolating nucleic acids from stool samples |
| WO2015023892A1 (en) | 2013-08-14 | 2015-02-19 | Gen-Probe Incorporated | Compositions and methods for detecting hev nucleic acid |
Family Cites Families (16)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| JPS6147500A (ja) | 1984-08-15 | 1986-03-07 | Res Dev Corp Of Japan | キメラモノクロ−ナル抗体及びその製造法 |
| EP0173494A3 (de) | 1984-08-27 | 1987-11-25 | The Board Of Trustees Of The Leland Stanford Junior University | Chimäre Rezeptoren durch Verbindung und Expression von DNS |
| GB8422238D0 (en) | 1984-09-03 | 1984-10-10 | Neuberger M S | Chimeric proteins |
| JPS61134325A (ja) | 1984-12-04 | 1986-06-21 | Teijin Ltd | ハイブリツド抗体遺伝子の発現方法 |
| US5741490A (en) * | 1988-06-17 | 1998-04-21 | Genelabs Technologies, Inc. | Hepatitis E virus vaccine and method |
| US5885768A (en) * | 1988-06-17 | 1999-03-23 | The United States Of America As Represented By The Department Of Health And Human Services | Hepatitis E virus peptide antigen and antibodies |
| US6455492B1 (en) * | 1988-06-17 | 2002-09-24 | Genelabs Technologies, Inc. | Hepatitis E virus vaccine and method |
| US6214970B1 (en) * | 1988-06-17 | 2001-04-10 | Genelabs Technologies, Inc. | Hepatitis E virus antigens and uses therefor |
| US5686239A (en) * | 1988-06-17 | 1997-11-11 | Genelabs Technologies, Inc. | Hepatitis E virus peptides and methods |
| EP0440663A1 (de) | 1988-08-08 | 1991-08-14 | IFFIU, Michael A. | Klappbares sesselrad mit stromlinienförmiger, in drei geteilter und faltbarer verkleidung |
| CA2016841C (en) | 1989-05-16 | 1999-09-21 | William D. Huse | A method for producing polymers having a preselected activity |
| ATE400658T1 (de) * | 1990-04-05 | 2008-07-15 | Genelabs Tech Inc | Enterisch übertragendes non-a/non-b-hepatitis- virus agens und charakteristische epitope von selbigem |
| WO1994006913A2 (en) * | 1992-09-18 | 1994-03-31 | The Government Of The United States Of America As Represented By The Secretary, Department Of Healthand Human Services | Recombinant proteins of a pakistani strain of hepatitis e and their use in diagnostic methods and vaccines |
| JPH09503912A (ja) * | 1993-09-24 | 1997-04-22 | ザ・マックファーレイン・バーネット・センター・フォー・メディカル・リサーチ・リミテッド | E型肝炎ウイルスの免疫反応性抗原 |
| CA2179609A1 (en) * | 1993-12-22 | 1995-06-29 | Deborah A. Paul | Monoclonal antibodies against hev orf-2 and methods for using same |
| KR100359526B1 (ko) * | 1994-10-03 | 2003-02-25 | 더 가브먼트 오브 더 유나이티드 스테이츠 오브 아메리카, 리프리젠티드 바이 더 세크러테리, 디파트먼트 오브 헬쓰 앤드 휴먼 서비씨즈 | E형간염파키스탄형균주의재조합단백질및이를이용한진단방법과백신 |
-
1997
- 1997-04-11 US US08/840,316 patent/US6054567A/en not_active Expired - Lifetime
-
1998
- 1998-04-09 AU AU72470/98A patent/AU739915B2/en not_active Ceased
- 1998-04-09 DE DE69839242T patent/DE69839242T2/de not_active Expired - Lifetime
- 1998-04-09 AT AT98919756T patent/ATE389021T1/de not_active IP Right Cessation
- 1998-04-09 CA CA002286399A patent/CA2286399C/en not_active Expired - Fee Related
- 1998-04-09 JP JP54417498A patent/JP4390293B2/ja not_active Expired - Fee Related
- 1998-04-09 WO PCT/US1998/007418 patent/WO1998046761A1/en active IP Right Grant
- 1998-04-09 ES ES98919756T patent/ES2301195T3/es not_active Expired - Lifetime
- 1998-04-09 EP EP08004467A patent/EP1958958B1/de not_active Expired - Lifetime
- 1998-04-09 EP EP98919756A patent/EP0972048B1/de not_active Expired - Lifetime
- 1998-04-09 AT AT08004467T patent/ATE530563T1/de not_active IP Right Cessation
- 1998-04-09 CN CNB988060353A patent/CN1202252C/zh not_active Expired - Fee Related
Also Published As
| Publication number | Publication date |
|---|---|
| US6054567A (en) | 2000-04-25 |
| EP0972048A1 (de) | 2000-01-19 |
| EP0972048B1 (de) | 2008-03-12 |
| CN1260000A (zh) | 2000-07-12 |
| CN1202252C (zh) | 2005-05-18 |
| AU7247098A (en) | 1998-11-11 |
| AU739915B2 (en) | 2001-10-25 |
| ATE389021T1 (de) | 2008-03-15 |
| JP2001524821A (ja) | 2001-12-04 |
| CA2286399A1 (en) | 1998-10-22 |
| DE69839242D1 (de) | 2008-04-24 |
| JP4390293B2 (ja) | 2009-12-24 |
| EP1958958B1 (de) | 2011-10-26 |
| ES2301195T3 (es) | 2008-06-16 |
| CA2286399C (en) | 2009-06-30 |
| WO1998046761A1 (en) | 1998-10-22 |
| ATE530563T1 (de) | 2011-11-15 |
| EP1958958A1 (de) | 2008-08-20 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| KR100318516B1 (ko) | E형 간염 파키스탄형 균주의 재조합 단백질 및 이를이용한 진단방법과 백신 | |
| DE69333859T2 (de) | Sich selbst-zusammenbauende rekombinante hpv16 papillomavirus hüllproteine | |
| DE3788902T3 (de) | Hepatitis-Delta-Diagnostika und Impfstoffe, ihre Herstellung und Verwendung. | |
| AT400724B (de) | Virales polypeptid | |
| DE69131882T3 (de) | Asiloglycoproteine des hepatitis c-virus | |
| DE69938062T2 (de) | Modifizierte hiv env polypeptide | |
| DE69934583T2 (de) | Nukleinsäure-impfstoffe zur verhinderung der flaviviren-infektion | |
| JPH05262667A (ja) | ウイルス抗原を用いるワクチン | |
| JPH0586088A (ja) | ニワトリ貧血ウイルスワクチン及び診断法 | |
| DE69533067T2 (de) | Hepatis e-virus antigene und dessen verwendungen | |
| DE69531308T2 (de) | Verfahren zur Herstellung von gereinigten papillomavirus Proteinen | |
| DE69839242T2 (de) | Rrekombinante proteine eines pakistani-stammes von hepatitis-e-virus, ihre verwendung in diagnotischen verfahren und als impfstoff | |
| KR100359526B1 (ko) | E형간염파키스탄형균주의재조합단백질및이를이용한진단방법과백신 | |
| DE69534242T2 (de) | Hämorrhagie-Virus | |
| DE60217129T2 (de) | Chimärische nukleinsäuren kodierend für proteine, die effekte gegen viren induzieren | |
| WO1998023754A1 (es) | Procedimiento para la expresion de genes de los virus del dengue | |
| US6458562B1 (en) | Recombinant proteins of a Pakistani strain of hepatitis E and their use in diagnostic methods and vaccines | |
| DE60028365T2 (de) | Chimäre nukleinsäuren und polypeptide aus lyssavirus | |
| DE60120391T2 (de) | Verwendung von hev-polypeptiden | |
| DE69133382T3 (de) | Asialoglycoproteine des Hepatitis C-Virus | |
| AU2010212374A1 (en) | Recombinant proteins of a Pakistani strain of hepatitis E and their use in diagnostic methods and vaccines | |
| US6491921B1 (en) | Avian polyomavirus vaccines in psittacine birds | |
| CA2201588A1 (en) | Recombinant proteins of a pakistani strain of hepatitis e and their use in diagnostic methods and vaccines |
Legal Events
| Date | Code | Title | Description |
|---|---|---|---|
| 8364 | No opposition during term of opposition | ||
| R082 | Change of representative |
Ref document number: 972048 Country of ref document: EP Representative=s name: DR. VOLKER VOSSIUS, CORINNA VOSSIUS, TILMAN VO, DE |
|
| R081 | Change of applicant/patentee |
Ref document number: 972048 Country of ref document: EP Owner name: NOVAVAX, INC., US Free format text: FORMER OWNER: THE GOVERNMENT OF THE UNITED STATES OF AMERICA AS REPRESENTED BY THE SECRETARY, DEPARTMENT OF HEALTH AND HUMAN SERVICES, ROCKVILLE, US Effective date: 20120824 Ref document number: 972048 Country of ref document: EP Owner name: THE GOVERNMENT OF THE UNITED STATES OF AMERICA, US Free format text: FORMER OWNER: THE GOVERNMENT OF THE UNITED STATES OF AMERICA AS REPRESENTED BY THE SECRETARY, DEPARTMENT OF HEALTH AND HUMAN SERVICES, ROCKVILLE, US Effective date: 20120824 |
|
| R082 | Change of representative |
Ref document number: 972048 Country of ref document: EP Representative=s name: DR. VOLKER VOSSIUS, CORINNA VOSSIUS, TILMAN VO, DE Effective date: 20120824 |