JP6847036B2 - アセトインを産生する方法 - Google Patents
アセトインを産生する方法 Download PDFInfo
- Publication number
- JP6847036B2 JP6847036B2 JP2017524104A JP2017524104A JP6847036B2 JP 6847036 B2 JP6847036 B2 JP 6847036B2 JP 2017524104 A JP2017524104 A JP 2017524104A JP 2017524104 A JP2017524104 A JP 2017524104A JP 6847036 B2 JP6847036 B2 JP 6847036B2
- Authority
- JP
- Japan
- Prior art keywords
- gene
- als
- sequence
- nucleic acid
- ald
- Prior art date
- Legal status (The legal status is an assumption and is not a legal conclusion. Google has not performed a legal analysis and makes no representation as to the accuracy of the status listed.)
- Active
Links
- ROWKJAVDOGWPAT-UHFFFAOYSA-N Acetoin Chemical compound CC(O)C(C)=O ROWKJAVDOGWPAT-UHFFFAOYSA-N 0.000 title claims description 175
- GFAZHVHNLUBROE-UHFFFAOYSA-N hydroxymethyl propionaldehyde Natural products CCC(=O)CO GFAZHVHNLUBROE-UHFFFAOYSA-N 0.000 title claims description 86
- 108090000623 proteins and genes Proteins 0.000 claims description 272
- 240000004808 Saccharomyces cerevisiae Species 0.000 claims description 207
- 235000014680 Saccharomyces cerevisiae Nutrition 0.000 claims description 202
- 150000007523 nucleic acids Chemical class 0.000 claims description 176
- 108020004414 DNA Proteins 0.000 claims description 157
- 108010000700 Acetolactate synthase Proteins 0.000 claims description 143
- 108020004707 nucleic acids Proteins 0.000 claims description 143
- 102000039446 nucleic acids Human genes 0.000 claims description 143
- 108010007843 NADH oxidase Proteins 0.000 claims description 139
- 108010084631 acetolactate decarboxylase Proteins 0.000 claims description 121
- 230000014509 gene expression Effects 0.000 claims description 84
- 230000000694 effects Effects 0.000 claims description 50
- 238000000034 method Methods 0.000 claims description 48
- 101150050575 URA3 gene Proteins 0.000 claims description 45
- 108010011939 Pyruvate Decarboxylase Proteins 0.000 claims description 44
- 238000004519 manufacturing process Methods 0.000 claims description 41
- 238000013518 transcription Methods 0.000 claims description 38
- 230000035897 transcription Effects 0.000 claims description 37
- 239000001963 growth medium Substances 0.000 claims description 34
- 230000002829 reductive effect Effects 0.000 claims description 32
- 108700007698 Genetic Terminator Regions Proteins 0.000 claims description 27
- OKTJSMMVPCPJKN-UHFFFAOYSA-N Carbon Chemical compound [C] OKTJSMMVPCPJKN-UHFFFAOYSA-N 0.000 claims description 24
- 229910052799 carbon Inorganic materials 0.000 claims description 24
- 230000001105 regulatory effect Effects 0.000 claims description 23
- 108091028043 Nucleic acid sequence Proteins 0.000 claims description 21
- 101150034686 PDC gene Proteins 0.000 claims description 18
- FUSUHKVFWTUUBE-UHFFFAOYSA-N buten-2-one Chemical compound CC(=O)C=C FUSUHKVFWTUUBE-UHFFFAOYSA-N 0.000 claims description 14
- 230000037431 insertion Effects 0.000 claims description 13
- 238000003780 insertion Methods 0.000 claims description 13
- 238000012258 culturing Methods 0.000 claims description 6
- 150000001413 amino acids Chemical group 0.000 description 49
- 244000005700 microbiome Species 0.000 description 49
- 230000036961 partial effect Effects 0.000 description 44
- SRBFZHDQGSBBOR-IOVATXLUSA-N D-xylopyranose Chemical compound O[C@@H]1COC(O)[C@H](O)[C@H]1O SRBFZHDQGSBBOR-IOVATXLUSA-N 0.000 description 40
- 101100246753 Halobacterium salinarum (strain ATCC 700922 / JCM 11081 / NRC-1) pyrF gene Proteins 0.000 description 40
- 238000000231 atomic layer deposition Methods 0.000 description 38
- 102000004190 Enzymes Human genes 0.000 description 37
- 108090000790 Enzymes Proteins 0.000 description 37
- 101100028920 Neurospora crassa (strain ATCC 24698 / 74-OR23-1A / CBS 708.71 / DSM 1257 / FGSC 987) cfp gene Proteins 0.000 description 37
- 229940088598 enzyme Drugs 0.000 description 37
- 210000004027 cell Anatomy 0.000 description 34
- PYMYPHUHKUWMLA-UHFFFAOYSA-N arabinose Natural products OCC(O)C(O)C(O)C=O PYMYPHUHKUWMLA-UHFFFAOYSA-N 0.000 description 31
- SRBFZHDQGSBBOR-UHFFFAOYSA-N beta-D-Pyranose-Lyxose Natural products OC1COC(O)C(O)C1O SRBFZHDQGSBBOR-UHFFFAOYSA-N 0.000 description 31
- LFQSCWFLJHTTHZ-UHFFFAOYSA-N Ethanol Chemical compound CCO LFQSCWFLJHTTHZ-UHFFFAOYSA-N 0.000 description 30
- -1 AURl-C Proteins 0.000 description 29
- WQZGKKKJIJFFOK-GASJEMHNSA-N Glucose Natural products OC[C@H]1OC(O)[C@H](O)[C@@H](O)[C@@H]1O WQZGKKKJIJFFOK-GASJEMHNSA-N 0.000 description 29
- 238000000855 fermentation Methods 0.000 description 29
- 230000004151 fermentation Effects 0.000 description 29
- 239000008103 glucose Substances 0.000 description 27
- 101150009006 HIS3 gene Proteins 0.000 description 26
- 101100394989 Rhodopseudomonas palustris (strain ATCC BAA-98 / CGA009) hisI gene Proteins 0.000 description 26
- 101150006914 TRP1 gene Proteins 0.000 description 25
- 239000002773 nucleotide Substances 0.000 description 25
- 125000003729 nucleotide group Chemical group 0.000 description 25
- 229940024606 amino acid Drugs 0.000 description 21
- 239000000203 mixture Substances 0.000 description 18
- 230000002018 overexpression Effects 0.000 description 17
- 239000000047 product Substances 0.000 description 17
- 239000000758 substrate Substances 0.000 description 17
- 230000012010 growth Effects 0.000 description 16
- 230000000813 microbial effect Effects 0.000 description 16
- 101150051897 his5 gene Proteins 0.000 description 15
- 108091026890 Coding region Proteins 0.000 description 13
- 235000000346 sugar Nutrition 0.000 description 13
- 241000235070 Saccharomyces Species 0.000 description 12
- 229930006000 Sucrose Natural products 0.000 description 12
- 239000003550 marker Substances 0.000 description 12
- 239000002609 medium Substances 0.000 description 12
- 239000005720 sucrose Substances 0.000 description 12
- CZMRCDWAGMRECN-UGDNZRGBSA-N Sucrose Chemical compound O[C@H]1[C@H](O)[C@@H](CO)O[C@@]1(CO)O[C@@H]1[C@H](O)[C@@H](O)[C@H](O)[C@@H](CO)O1 CZMRCDWAGMRECN-UGDNZRGBSA-N 0.000 description 11
- 102000004169 proteins and genes Human genes 0.000 description 11
- IJGRMHOSHXDMSA-UHFFFAOYSA-N Atomic nitrogen Chemical compound N#N IJGRMHOSHXDMSA-UHFFFAOYSA-N 0.000 description 10
- 241000894006 Bacteria Species 0.000 description 10
- 101150101337 Bdh2 gene Proteins 0.000 description 10
- PYMYPHUHKUWMLA-WDCZJNDASA-N arabinose Chemical compound OC[C@@H](O)[C@@H](O)[C@H](O)C=O PYMYPHUHKUWMLA-WDCZJNDASA-N 0.000 description 10
- 238000006243 chemical reaction Methods 0.000 description 10
- BOPGDPNILDQYTO-NNYOXOHSSA-N nicotinamide-adenine dinucleotide Chemical compound C1=CCC(C(=O)N)=CN1[C@H]1[C@H](O)[C@H](O)[C@@H](COP(O)(=O)OP(O)(=O)OC[C@@H]2[C@H]([C@@H](O)[C@@H](O2)N2C3=NC=NC(N)=C3N=C2)O)O1 BOPGDPNILDQYTO-NNYOXOHSSA-N 0.000 description 10
- 230000015572 biosynthetic process Effects 0.000 description 9
- 210000005253 yeast cell Anatomy 0.000 description 9
- 230000035772 mutation Effects 0.000 description 8
- 229910052760 oxygen Inorganic materials 0.000 description 8
- 229940076788 pyruvate Drugs 0.000 description 8
- NMDWGEGFJUBKLB-YFKPBYRVSA-N (2S)-2-hydroxy-2-methyl-3-oxobutanoic acid Chemical compound CC(=O)[C@](C)(O)C(O)=O NMDWGEGFJUBKLB-YFKPBYRVSA-N 0.000 description 7
- 101150021974 Adh1 gene Proteins 0.000 description 7
- 102000004031 Carboxy-Lyases Human genes 0.000 description 7
- 102000004316 Oxidoreductases Human genes 0.000 description 7
- 108090000854 Oxidoreductases Proteins 0.000 description 7
- LCTONWCANYUPML-UHFFFAOYSA-M Pyruvate Chemical compound CC(=O)C([O-])=O LCTONWCANYUPML-UHFFFAOYSA-M 0.000 description 7
- 239000002253 acid Substances 0.000 description 7
- QVGXLLKOCUKJST-UHFFFAOYSA-N atomic oxygen Chemical compound [O] QVGXLLKOCUKJST-UHFFFAOYSA-N 0.000 description 7
- 229940041514 candida albicans extract Drugs 0.000 description 7
- 230000001965 increasing effect Effects 0.000 description 7
- 229930027945 nicotinamide-adenine dinucleotide Natural products 0.000 description 7
- 239000001301 oxygen Substances 0.000 description 7
- 238000003786 synthesis reaction Methods 0.000 description 7
- 239000012138 yeast extract Substances 0.000 description 7
- FQVLRGLGWNWPSS-BXBUPLCLSA-N (4r,7s,10s,13s,16r)-16-acetamido-13-(1h-imidazol-5-ylmethyl)-10-methyl-6,9,12,15-tetraoxo-7-propan-2-yl-1,2-dithia-5,8,11,14-tetrazacycloheptadecane-4-carboxamide Chemical group N1C(=O)[C@@H](NC(C)=O)CSSC[C@@H](C(N)=O)NC(=O)[C@H](C(C)C)NC(=O)[C@H](C)NC(=O)[C@@H]1CC1=CN=CN1 FQVLRGLGWNWPSS-BXBUPLCLSA-N 0.000 description 6
- CURLTUGMZLYLDI-UHFFFAOYSA-N Carbon dioxide Chemical compound O=C=O CURLTUGMZLYLDI-UHFFFAOYSA-N 0.000 description 6
- PEDCQBHIVMGVHV-UHFFFAOYSA-N Glycerine Chemical compound OCC(O)CO PEDCQBHIVMGVHV-UHFFFAOYSA-N 0.000 description 6
- 210000000349 chromosome Anatomy 0.000 description 6
- 230000007613 environmental effect Effects 0.000 description 6
- 239000013612 plasmid Substances 0.000 description 6
- AXPZIVKEZRHGAS-UHFFFAOYSA-N 3-benzyl-5-[(2-nitrophenoxy)methyl]oxolan-2-one Chemical compound [O-][N+](=O)C1=CC=CC=C1OCC1OC(=O)C(CC=2C=CC=CC=2)C1 AXPZIVKEZRHGAS-UHFFFAOYSA-N 0.000 description 5
- 101100001031 Acetobacter aceti adhA gene Proteins 0.000 description 5
- 101710088194 Dehydrogenase Proteins 0.000 description 5
- 101100054935 Emericella nidulans (strain FGSC A4 / ATCC 38163 / CBS 112.46 / NRRL 194 / M139) alcC gene Proteins 0.000 description 5
- 230000001195 anabolic effect Effects 0.000 description 5
- 230000001580 bacterial effect Effects 0.000 description 5
- WQZGKKKJIJFFOK-VFUOTHLCSA-N beta-D-glucose Chemical compound OC[C@H]1O[C@@H](O)[C@H](O)[C@@H](O)[C@@H]1O WQZGKKKJIJFFOK-VFUOTHLCSA-N 0.000 description 5
- 230000002759 chromosomal effect Effects 0.000 description 5
- 230000037430 deletion Effects 0.000 description 5
- 238000012217 deletion Methods 0.000 description 5
- 238000005516 engineering process Methods 0.000 description 5
- 230000002068 genetic effect Effects 0.000 description 5
- 230000010354 integration Effects 0.000 description 5
- 230000004060 metabolic process Effects 0.000 description 5
- 230000004048 modification Effects 0.000 description 5
- 238000012986 modification Methods 0.000 description 5
- 229910052757 nitrogen Inorganic materials 0.000 description 5
- 235000015097 nutrients Nutrition 0.000 description 5
- 230000037361 pathway Effects 0.000 description 5
- 238000000746 purification Methods 0.000 description 5
- 238000010561 standard procedure Methods 0.000 description 5
- 101001058938 Acidaminococcus fermentans (strain ATCC 25085 / DSM 20731 / CCUG 9996 / CIP 106432 / VR4) Glutaconyl-CoA decarboxylase subunit beta Proteins 0.000 description 4
- 229930024421 Adenine Natural products 0.000 description 4
- GFFGJBXGBJISGV-UHFFFAOYSA-N Adenine Chemical compound NC1=NC=NC2=C1N=CN2 GFFGJBXGBJISGV-UHFFFAOYSA-N 0.000 description 4
- 108091029865 Exogenous DNA Proteins 0.000 description 4
- BAWFJGJZGIEFAR-NNYOXOHSSA-N NAD zwitterion Chemical compound NC(=O)C1=CC=C[N+]([C@H]2[C@@H]([C@H](O)[C@@H](COP([O-])(=O)OP(O)(=O)OC[C@@H]3[C@H]([C@@H](O)[C@@H](O3)N3C4=NC=NC(N)=C4N=C3)O)O2)O)=C1 BAWFJGJZGIEFAR-NNYOXOHSSA-N 0.000 description 4
- OFBQJSOFQDEBGM-UHFFFAOYSA-N Pentane Chemical compound CCCCC OFBQJSOFQDEBGM-UHFFFAOYSA-N 0.000 description 4
- LCTONWCANYUPML-UHFFFAOYSA-N Pyruvic acid Chemical compound CC(=O)C(O)=O LCTONWCANYUPML-UHFFFAOYSA-N 0.000 description 4
- 150000007513 acids Chemical class 0.000 description 4
- 229960000643 adenine Drugs 0.000 description 4
- 230000004077 genetic alteration Effects 0.000 description 4
- 231100000118 genetic alteration Toxicity 0.000 description 4
- JVTAAEKCZFNVCJ-UHFFFAOYSA-N lactic acid Chemical compound CC(O)C(O)=O JVTAAEKCZFNVCJ-UHFFFAOYSA-N 0.000 description 4
- 239000002207 metabolite Substances 0.000 description 4
- 230000008569 process Effects 0.000 description 4
- QTBSBXVTEAMEQO-UHFFFAOYSA-N Acetic acid Chemical compound CC(O)=O QTBSBXVTEAMEQO-UHFFFAOYSA-N 0.000 description 3
- 108010021809 Alcohol dehydrogenase Proteins 0.000 description 3
- 102000007698 Alcohol dehydrogenase Human genes 0.000 description 3
- 101100272861 Arabidopsis thaliana BXL3 gene Proteins 0.000 description 3
- 108010023063 Bacto-peptone Proteins 0.000 description 3
- UHOVQNZJYSORNB-UHFFFAOYSA-N Benzene Chemical compound C1=CC=CC=C1 UHOVQNZJYSORNB-UHFFFAOYSA-N 0.000 description 3
- 241000722885 Brettanomyces Species 0.000 description 3
- 241000222120 Candida <Saccharomycetales> Species 0.000 description 3
- 108090000489 Carboxy-Lyases Proteins 0.000 description 3
- RTZKZFJDLAIYFH-UHFFFAOYSA-N Diethyl ether Chemical compound CCOCC RTZKZFJDLAIYFH-UHFFFAOYSA-N 0.000 description 3
- 241000588724 Escherichia coli Species 0.000 description 3
- 102000001390 Fructose-Bisphosphate Aldolase Human genes 0.000 description 3
- 108010068561 Fructose-Bisphosphate Aldolase Proteins 0.000 description 3
- GUBGYTABKSRVRQ-QKKXKWKRSA-N Lactose Natural products OC[C@H]1O[C@@H](O[C@H]2[C@H](O)[C@@H](O)C(O)O[C@@H]2CO)[C@H](O)[C@@H](O)[C@H]1O GUBGYTABKSRVRQ-QKKXKWKRSA-N 0.000 description 3
- 108010002998 NADPH Oxidases Proteins 0.000 description 3
- 102000004722 NADPH Oxidases Human genes 0.000 description 3
- 244000061176 Nicotiana tabacum Species 0.000 description 3
- 235000002637 Nicotiana tabacum Nutrition 0.000 description 3
- 241000235648 Pichia Species 0.000 description 3
- 241000235343 Saccharomycetales Species 0.000 description 3
- 229920002472 Starch Polymers 0.000 description 3
- YXFVVABEGXRONW-UHFFFAOYSA-N Toluene Chemical compound CC1=CC=CC=C1 YXFVVABEGXRONW-UHFFFAOYSA-N 0.000 description 3
- 241000235006 Torulaspora Species 0.000 description 3
- 101150100773 XKS1 gene Proteins 0.000 description 3
- 101150032931 XYL3 gene Proteins 0.000 description 3
- 239000000370 acceptor Substances 0.000 description 3
- 230000003115 biocidal effect Effects 0.000 description 3
- 230000033228 biological regulation Effects 0.000 description 3
- 239000001569 carbon dioxide Substances 0.000 description 3
- 229910002092 carbon dioxide Inorganic materials 0.000 description 3
- 239000001913 cellulose Substances 0.000 description 3
- 229920002678 cellulose Polymers 0.000 description 3
- 230000000295 complement effect Effects 0.000 description 3
- 238000004821 distillation Methods 0.000 description 3
- 238000000605 extraction Methods 0.000 description 3
- 239000000796 flavoring agent Substances 0.000 description 3
- 239000007789 gas Substances 0.000 description 3
- 238000012239 gene modification Methods 0.000 description 3
- 230000005017 genetic modification Effects 0.000 description 3
- 235000013617 genetically modified food Nutrition 0.000 description 3
- 239000004615 ingredient Substances 0.000 description 3
- 239000008101 lactose Substances 0.000 description 3
- 239000007788 liquid Substances 0.000 description 3
- VLKZOEOYAKHREP-UHFFFAOYSA-N n-Hexane Chemical compound CCCCCC VLKZOEOYAKHREP-UHFFFAOYSA-N 0.000 description 3
- 230000002265 prevention Effects 0.000 description 3
- 229940107700 pyruvic acid Drugs 0.000 description 3
- 241000894007 species Species 0.000 description 3
- 239000008107 starch Substances 0.000 description 3
- 235000019698 starch Nutrition 0.000 description 3
- 239000000126 substance Substances 0.000 description 3
- 238000013519 translation Methods 0.000 description 3
- 238000011144 upstream manufacturing Methods 0.000 description 3
- RLMLFADXHJLPSQ-NPPFTVEMSA-N (3s,6s,9s,12s,15s,18s,21s,24r,27s)-3,6-dibenzyl-12,24-bis[(2r)-butan-2-yl]-15-(2-hydroxypropan-2-yl)-4,10,16,22-tetramethyl-18-(2-methylpropyl)-9,21-di(propan-2-yl)-13-oxa-1,4,7,10,16,19,22,25-octazabicyclo[25.3.0]triacontane-2,5,8,11,14,17,20,23,26-nonon Chemical compound C([C@H]1C(=O)N2CCC[C@H]2C(=O)N[C@@H](C(N(C)[C@@H](C(C)C)C(=O)N[C@@H](CC(C)C)C(=O)N(C)[C@H](C(=O)O[C@H](C(=O)N(C)[C@@H](C(C)C)C(=O)N[C@@H](CC=2C=CC=CC=2)C(=O)N1C)[C@H](C)CC)C(C)(C)O)=O)[C@H](C)CC)C1=CC=CC=C1 RLMLFADXHJLPSQ-NPPFTVEMSA-N 0.000 description 2
- OWEGMIWEEQEYGQ-UHFFFAOYSA-N 100676-05-9 Natural products OC1C(O)C(O)C(CO)OC1OCC1C(O)C(O)C(O)C(OC2C(OC(O)C(O)C2O)CO)O1 OWEGMIWEEQEYGQ-UHFFFAOYSA-N 0.000 description 2
- KMZHZAAOEWVPSE-UHFFFAOYSA-N 2,3-dihydroxypropyl acetate Chemical compound CC(=O)OCC(O)CO KMZHZAAOEWVPSE-UHFFFAOYSA-N 0.000 description 2
- OSJPPGNTCRNQQC-UWTATZPHSA-N 3-phospho-D-glyceric acid Chemical compound OC(=O)[C@H](O)COP(O)(O)=O OSJPPGNTCRNQQC-UWTATZPHSA-N 0.000 description 2
- ZHBXLZQQVCDGPA-UHFFFAOYSA-N 5-[(1,3-dioxo-2-benzofuran-5-yl)sulfonyl]-2-benzofuran-1,3-dione Chemical compound C1=C2C(=O)OC(=O)C2=CC(S(=O)(=O)C=2C=C3C(=O)OC(C3=CC=2)=O)=C1 ZHBXLZQQVCDGPA-UHFFFAOYSA-N 0.000 description 2
- GUBGYTABKSRVRQ-XLOQQCSPSA-N Alpha-Lactose Chemical compound O[C@@H]1[C@@H](O)[C@@H](O)[C@@H](CO)O[C@H]1O[C@@H]1[C@@H](CO)O[C@H](O)[C@H](O)[C@H]1O GUBGYTABKSRVRQ-XLOQQCSPSA-N 0.000 description 2
- NLXLAEXVIDQMFP-UHFFFAOYSA-N Ammonia chloride Chemical compound [NH4+].[Cl-] NLXLAEXVIDQMFP-UHFFFAOYSA-N 0.000 description 2
- 101100272859 Arabidopsis thaliana BXL1 gene Proteins 0.000 description 2
- XKRFYHLGVUSROY-UHFFFAOYSA-N Argon Chemical compound [Ar] XKRFYHLGVUSROY-UHFFFAOYSA-N 0.000 description 2
- 101100264262 Aspergillus aculeatus xlnD gene Proteins 0.000 description 2
- 244000063299 Bacillus subtilis Species 0.000 description 2
- 235000014469 Bacillus subtilis Nutrition 0.000 description 2
- 241000193764 Brevibacillus brevis Species 0.000 description 2
- 241001508811 Clavispora Species 0.000 description 2
- 108020004705 Codon Proteins 0.000 description 2
- 108700010070 Codon Usage Proteins 0.000 description 2
- 241001337994 Cryptococcus <scale insect> Species 0.000 description 2
- ZAQJHHRNXZUBTE-WUJLRWPWSA-N D-xylulose Chemical compound OC[C@@H](O)[C@H](O)C(=O)CO ZAQJHHRNXZUBTE-WUJLRWPWSA-N 0.000 description 2
- 108010058076 D-xylulose reductase Proteins 0.000 description 2
- 108010083068 Dual Oxidases Proteins 0.000 description 2
- 102000006265 Dual Oxidases Human genes 0.000 description 2
- 101000904460 Encephalitozoon cuniculi (strain GB-M1) Probable glycerol-3-phosphate dehydrogenase Chemical group 0.000 description 2
- 101150095274 FBA1 gene Proteins 0.000 description 2
- 235000016623 Fragaria vesca Nutrition 0.000 description 2
- 240000009088 Fragaria x ananassa Species 0.000 description 2
- 235000011363 Fragaria x ananassa Nutrition 0.000 description 2
- 229930091371 Fructose Natural products 0.000 description 2
- 239000005715 Fructose Substances 0.000 description 2
- RFSUNEUAIZKAJO-ARQDHWQXSA-N Fructose Chemical compound OC[C@H]1O[C@](O)(CO)[C@@H](O)[C@@H]1O RFSUNEUAIZKAJO-ARQDHWQXSA-N 0.000 description 2
- 230000005526 G1 to G0 transition Effects 0.000 description 2
- 101100049998 Gibberella zeae (strain ATCC MYA-4620 / CBS 123657 / FGSC 9075 / NRRL 31084 / PH-1) XYLB gene Proteins 0.000 description 2
- 108010044467 Isoenzymes Proteins 0.000 description 2
- 101150037790 JEN1 gene Proteins 0.000 description 2
- 102000004317 Lyases Human genes 0.000 description 2
- 108090000856 Lyases Proteins 0.000 description 2
- GUBGYTABKSRVRQ-PICCSMPSSA-N Maltose Natural products O[C@@H]1[C@@H](O)[C@H](O)[C@@H](CO)O[C@@H]1O[C@@H]1[C@@H](CO)OC(O)[C@H](O)[C@H]1O GUBGYTABKSRVRQ-PICCSMPSSA-N 0.000 description 2
- LRHPLDYGYMQRHN-UHFFFAOYSA-N N-Butanol Chemical compound CCCCO LRHPLDYGYMQRHN-UHFFFAOYSA-N 0.000 description 2
- IMNFDUFMRHMDMM-UHFFFAOYSA-N N-Heptane Chemical compound CCCCCCC IMNFDUFMRHMDMM-UHFFFAOYSA-N 0.000 description 2
- 101150050255 PDC1 gene Proteins 0.000 description 2
- 241000179039 Paenibacillus Species 0.000 description 2
- 102000010292 Peptide Elongation Factor 1 Human genes 0.000 description 2
- 108010077524 Peptide Elongation Factor 1 Proteins 0.000 description 2
- 239000001888 Peptone Substances 0.000 description 2
- 108010080698 Peptones Proteins 0.000 description 2
- 108010022181 Phosphopyruvate Hydratase Proteins 0.000 description 2
- 102000012288 Phosphopyruvate Hydratase Human genes 0.000 description 2
- 102000001253 Protein Kinase Human genes 0.000 description 2
- 101100069420 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) GRE3 gene Proteins 0.000 description 2
- 101100507956 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) HXT7 gene Proteins 0.000 description 2
- 101100386089 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) MET17 gene Proteins 0.000 description 2
- 101100305145 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) RPP1A gene Proteins 0.000 description 2
- 241000235346 Schizosaccharomyces Species 0.000 description 2
- 102100026974 Sorbitol dehydrogenase Human genes 0.000 description 2
- 241000193998 Streptococcus pneumoniae Species 0.000 description 2
- 101150074253 TEF1 gene Chemical group 0.000 description 2
- 101150032817 TPI1 gene Proteins 0.000 description 2
- 102000005924 Triose-Phosphate Isomerase Human genes 0.000 description 2
- 108700015934 Triose-phosphate isomerases Proteins 0.000 description 2
- XSQUKJJJFZCRTK-UHFFFAOYSA-N Urea Chemical compound NC(N)=O XSQUKJJJFZCRTK-UHFFFAOYSA-N 0.000 description 2
- 101150095212 XYL2 gene Proteins 0.000 description 2
- TVXBFESIOXBWNM-UHFFFAOYSA-N Xylitol Natural products OCCC(O)C(O)C(O)CCO TVXBFESIOXBWNM-UHFFFAOYSA-N 0.000 description 2
- 102100029089 Xylulose kinase Human genes 0.000 description 2
- 238000009825 accumulation Methods 0.000 description 2
- ZSLZBFCDCINBPY-ZSJPKINUSA-N acetyl-CoA Chemical compound O[C@@H]1[C@H](OP(O)(O)=O)[C@@H](COP(O)(=O)OP(O)(=O)OCC(C)(C)[C@@H](O)C(=O)NCCC(=O)NCCSC(=O)C)O[C@H]1N1C2=NC=NC(N)=C2N=C1 ZSLZBFCDCINBPY-ZSJPKINUSA-N 0.000 description 2
- 238000007792 addition Methods 0.000 description 2
- 239000002386 air freshener Substances 0.000 description 2
- WQZGKKKJIJFFOK-PHYPRBDBSA-N alpha-D-galactose Chemical compound OC[C@H]1O[C@H](O)[C@H](O)[C@@H](O)[C@H]1O WQZGKKKJIJFFOK-PHYPRBDBSA-N 0.000 description 2
- 230000001668 ameliorated effect Effects 0.000 description 2
- BFNBIHQBYMNNAN-UHFFFAOYSA-N ammonium sulfate Chemical compound N.N.OS(O)(=O)=O BFNBIHQBYMNNAN-UHFFFAOYSA-N 0.000 description 2
- 229910052921 ammonium sulfate Inorganic materials 0.000 description 2
- 235000011130 ammonium sulphate Nutrition 0.000 description 2
- 230000002238 attenuated effect Effects 0.000 description 2
- 108010008887 aureobasidin A Proteins 0.000 description 2
- 101150038738 ble gene Proteins 0.000 description 2
- 230000003197 catalytic effect Effects 0.000 description 2
- 235000013351 cheese Nutrition 0.000 description 2
- 239000007795 chemical reaction product Substances 0.000 description 2
- 230000007812 deficiency Effects 0.000 description 2
- 230000001419 dependent effect Effects 0.000 description 2
- 239000008121 dextrose Substances 0.000 description 2
- SNRUBQQJIBEYMU-UHFFFAOYSA-N dodecane Chemical compound CCCCCCCCCCCC SNRUBQQJIBEYMU-UHFFFAOYSA-N 0.000 description 2
- 230000002708 enhancing effect Effects 0.000 description 2
- 101150104041 eno2 gene Proteins 0.000 description 2
- 235000019634 flavors Nutrition 0.000 description 2
- 235000013305 food Nutrition 0.000 description 2
- 229930182830 galactose Natural products 0.000 description 2
- 238000004817 gas chromatography Methods 0.000 description 2
- 101150087371 gpd1 gene Proteins 0.000 description 2
- 239000003102 growth factor Substances 0.000 description 2
- 235000015243 ice cream Nutrition 0.000 description 2
- 230000002779 inactivation Effects 0.000 description 2
- 230000005764 inhibitory process Effects 0.000 description 2
- 239000004310 lactic acid Substances 0.000 description 2
- 235000014655 lactic acid Nutrition 0.000 description 2
- 235000013310 margarine Nutrition 0.000 description 2
- 239000003264 margarine Substances 0.000 description 2
- HEBKCHPVOIAQTA-UHFFFAOYSA-N meso ribitol Natural products OCC(O)C(O)C(O)CO HEBKCHPVOIAQTA-UHFFFAOYSA-N 0.000 description 2
- 230000037353 metabolic pathway Effects 0.000 description 2
- 150000002772 monosaccharides Chemical class 0.000 description 2
- 238000002703 mutagenesis Methods 0.000 description 2
- 231100000350 mutagenesis Toxicity 0.000 description 2
- 239000006225 natural substrate Substances 0.000 description 2
- 229920001542 oligosaccharide Polymers 0.000 description 2
- 150000002482 oligosaccharides Chemical class 0.000 description 2
- 239000003960 organic solvent Substances 0.000 description 2
- 230000004108 pentose phosphate pathway Effects 0.000 description 2
- 150000002972 pentoses Chemical class 0.000 description 2
- 235000019319 peptone Nutrition 0.000 description 2
- 101150079312 pgk1 gene Proteins 0.000 description 2
- LWIHDJKSTIGBAC-UHFFFAOYSA-K potassium phosphate Substances [K+].[K+].[K+].[O-]P([O-])([O-])=O LWIHDJKSTIGBAC-UHFFFAOYSA-K 0.000 description 2
- 108060006633 protein kinase Proteins 0.000 description 2
- 230000009467 reduction Effects 0.000 description 2
- 238000011160 research Methods 0.000 description 2
- 150000003839 salts Chemical class 0.000 description 2
- 229940031000 streptococcus pneumoniae Drugs 0.000 description 2
- 150000008163 sugars Chemical class 0.000 description 2
- 210000001685 thyroid gland Anatomy 0.000 description 2
- 230000002103 transcriptional effect Effects 0.000 description 2
- 230000001131 transforming effect Effects 0.000 description 2
- XLYOFNOQVPJJNP-UHFFFAOYSA-N water Substances O XLYOFNOQVPJJNP-UHFFFAOYSA-N 0.000 description 2
- 101150034227 xyl1 gene Proteins 0.000 description 2
- 239000000811 xylitol Substances 0.000 description 2
- HEBKCHPVOIAQTA-SCDXWVJYSA-N xylitol Chemical compound OC[C@H](O)[C@@H](O)[C@H](O)CO HEBKCHPVOIAQTA-SCDXWVJYSA-N 0.000 description 2
- 229960002675 xylitol Drugs 0.000 description 2
- 235000010447 xylitol Nutrition 0.000 description 2
- 108091022915 xylulokinase Proteins 0.000 description 2
- PAWQVTBBRAZDMG-UHFFFAOYSA-N 2-(3-bromo-2-fluorophenyl)acetic acid Chemical compound OC(=O)CC1=CC=CC(Br)=C1F PAWQVTBBRAZDMG-UHFFFAOYSA-N 0.000 description 1
- MIDXCONKKJTLDX-UHFFFAOYSA-N 3,5-dimethylcyclopentane-1,2-dione Chemical compound CC1CC(C)C(=O)C1=O MIDXCONKKJTLDX-UHFFFAOYSA-N 0.000 description 1
- 101710163881 5,6-dihydroxyindole-2-carboxylic acid oxidase Proteins 0.000 description 1
- 101150096273 ADE2 gene Proteins 0.000 description 1
- 102100024643 ATP-binding cassette sub-family D member 1 Human genes 0.000 description 1
- QTBSBXVTEAMEQO-UHFFFAOYSA-M Acetate Chemical compound CC([O-])=O QTBSBXVTEAMEQO-UHFFFAOYSA-M 0.000 description 1
- 102100034035 Alcohol dehydrogenase 1A Human genes 0.000 description 1
- 239000004254 Ammonium phosphate Substances 0.000 description 1
- 241000219195 Arabidopsis thaliana Species 0.000 description 1
- 101100517196 Arabidopsis thaliana NRPE1 gene Proteins 0.000 description 1
- 101100374156 Arabidopsis thaliana RKL1 gene Proteins 0.000 description 1
- 101710129685 Arabinose-proton symporter Proteins 0.000 description 1
- 101100434663 Bacillus subtilis (strain 168) fbaA gene Proteins 0.000 description 1
- 102100030981 Beta-alanine-activating enzyme Human genes 0.000 description 1
- 239000002028 Biomass Substances 0.000 description 1
- 101100190825 Bos taurus PMEL gene Proteins 0.000 description 1
- 244000027711 Brettanomyces bruxellensis Species 0.000 description 1
- FERIUCNNQQJTOY-UHFFFAOYSA-M Butyrate Chemical compound CCCC([O-])=O FERIUCNNQQJTOY-UHFFFAOYSA-M 0.000 description 1
- 101100480861 Caldanaerobacter subterraneus subsp. tengcongensis (strain DSM 15242 / JCM 11007 / NBRC 100824 / MB4) tdh gene Proteins 0.000 description 1
- 101100351264 Candida albicans (strain SC5314 / ATCC MYA-2876) PDC11 gene Proteins 0.000 description 1
- 101100447466 Candida albicans (strain WO-1) TDH1 gene Proteins 0.000 description 1
- BVKZGUZCCUSVTD-UHFFFAOYSA-L Carbonate Chemical compound [O-]C([O-])=O BVKZGUZCCUSVTD-UHFFFAOYSA-L 0.000 description 1
- 108010078791 Carrier Proteins Proteins 0.000 description 1
- 244000060011 Cocos nucifera Species 0.000 description 1
- 235000013162 Cocos nucifera Nutrition 0.000 description 1
- 108091035707 Consensus sequence Proteins 0.000 description 1
- XDTMQSROBMDMFD-UHFFFAOYSA-N Cyclohexane Chemical compound C1CCCCC1 XDTMQSROBMDMFD-UHFFFAOYSA-N 0.000 description 1
- GUBGYTABKSRVRQ-CUHNMECISA-N D-Cellobiose Chemical compound O[C@@H]1[C@@H](O)[C@H](O)[C@@H](CO)O[C@H]1O[C@@H]1[C@@H](CO)OC(O)[C@H](O)[C@H]1O GUBGYTABKSRVRQ-CUHNMECISA-N 0.000 description 1
- MTCFGRXMJLQNBG-UWTATZPHSA-N D-Serine Chemical compound OC[C@@H](N)C(O)=O MTCFGRXMJLQNBG-UWTATZPHSA-N 0.000 description 1
- 229930195711 D-Serine Natural products 0.000 description 1
- RBNPOMFGQQGHHO-UWTATZPHSA-N D-glyceric acid Chemical compound OC[C@@H](O)C(O)=O RBNPOMFGQQGHHO-UWTATZPHSA-N 0.000 description 1
- WQZGKKKJIJFFOK-QTVWNMPRSA-N D-mannopyranose Chemical compound OC[C@H]1OC(O)[C@@H](O)[C@@H](O)[C@@H]1O WQZGKKKJIJFFOK-QTVWNMPRSA-N 0.000 description 1
- ZAQJHHRNXZUBTE-NQXXGFSBSA-N D-ribulose Chemical compound OC[C@@H](O)[C@@H](O)C(=O)CO ZAQJHHRNXZUBTE-NQXXGFSBSA-N 0.000 description 1
- ZAQJHHRNXZUBTE-UHFFFAOYSA-N D-threo-2-Pentulose Natural products OCC(O)C(O)C(=O)CO ZAQJHHRNXZUBTE-UHFFFAOYSA-N 0.000 description 1
- FNZLKVNUWIIPSJ-RFZPGFLSSA-N D-xylulose 5-phosphate Chemical compound OCC(=O)[C@@H](O)[C@H](O)COP(O)(O)=O FNZLKVNUWIIPSJ-RFZPGFLSSA-N 0.000 description 1
- 241000235035 Debaryomyces Species 0.000 description 1
- QSJXEFYPDANLFS-UHFFFAOYSA-N Diacetyl Chemical group CC(=O)C(C)=O QSJXEFYPDANLFS-UHFFFAOYSA-N 0.000 description 1
- MYMOFIZGZYHOMD-UHFFFAOYSA-N Dioxygen Chemical compound O=O MYMOFIZGZYHOMD-UHFFFAOYSA-N 0.000 description 1
- 102100021217 Dual oxidase 2 Human genes 0.000 description 1
- 241000196324 Embryophyta Species 0.000 description 1
- 241000588914 Enterobacter Species 0.000 description 1
- 241000194032 Enterococcus faecalis Species 0.000 description 1
- 241001465321 Eremothecium Species 0.000 description 1
- 241000233866 Fungi Species 0.000 description 1
- 101150037782 GAL2 gene Proteins 0.000 description 1
- 101150081655 GPM1 gene Proteins 0.000 description 1
- 102100023413 GRB2-related adapter protein Human genes 0.000 description 1
- 102100021735 Galectin-2 Human genes 0.000 description 1
- 101000892220 Geobacillus thermodenitrificans (strain NG80-2) Long-chain-alcohol dehydrogenase 1 Proteins 0.000 description 1
- 108010073178 Glucan 1,4-alpha-Glucosidase Proteins 0.000 description 1
- 102100022624 Glucoamylase Human genes 0.000 description 1
- 102100036669 Glycerol-3-phosphate dehydrogenase [NAD(+)], cytoplasmic Human genes 0.000 description 1
- 108010041921 Glycerolphosphate Dehydrogenase Proteins 0.000 description 1
- 101150044896 HXT4 gene Proteins 0.000 description 1
- 102000002812 Heat-Shock Proteins Human genes 0.000 description 1
- 108010004889 Heat-Shock Proteins Proteins 0.000 description 1
- 229920002488 Hemicellulose Polymers 0.000 description 1
- 101000780443 Homo sapiens Alcohol dehydrogenase 1A Proteins 0.000 description 1
- 101000884385 Homo sapiens Arylamine N-acetyltransferase 1 Proteins 0.000 description 1
- 101000773364 Homo sapiens Beta-alanine-activating enzyme Proteins 0.000 description 1
- 101000968305 Homo sapiens Dual oxidase 2 Proteins 0.000 description 1
- 101001034811 Homo sapiens Eukaryotic translation initiation factor 4 gamma 2 Proteins 0.000 description 1
- 101000829735 Homo sapiens GRB2-related adapter protein Proteins 0.000 description 1
- 101001012669 Homo sapiens Melanoma inhibitory activity protein 2 Proteins 0.000 description 1
- 101000601616 Homo sapiens NADH dehydrogenase [ubiquinone] 1 alpha subcomplex subunit 1 Proteins 0.000 description 1
- 101001128581 Homo sapiens NADH dehydrogenase [ubiquinone] 1 alpha subcomplex subunit 5 Proteins 0.000 description 1
- 101000579123 Homo sapiens Phosphoglycerate kinase 1 Proteins 0.000 description 1
- 101000639975 Homo sapiens Sodium-dependent noradrenaline transporter Proteins 0.000 description 1
- 240000005979 Hordeum vulgare Species 0.000 description 1
- 235000007340 Hordeum vulgare Nutrition 0.000 description 1
- 108010020056 Hydrogenase Proteins 0.000 description 1
- 102000004195 Isomerases Human genes 0.000 description 1
- 108090000769 Isomerases Proteins 0.000 description 1
- 240000007049 Juglans regia Species 0.000 description 1
- 235000009496 Juglans regia Nutrition 0.000 description 1
- 241000588915 Klebsiella aerogenes Species 0.000 description 1
- 201000008225 Klebsiella pneumonia Diseases 0.000 description 1
- 241000588747 Klebsiella pneumoniae Species 0.000 description 1
- 241000235649 Kluyveromyces Species 0.000 description 1
- 241001138401 Kluyveromyces lactis Species 0.000 description 1
- HEBKCHPVOIAQTA-IMJSIDKUSA-N L-arabinitol Chemical compound OC[C@H](O)C(O)[C@@H](O)CO HEBKCHPVOIAQTA-IMJSIDKUSA-N 0.000 description 1
- AGPKZVBTJJNPAG-WHFBIAKZSA-N L-isoleucine Chemical compound CC[C@H](C)[C@H](N)C(O)=O AGPKZVBTJJNPAG-WHFBIAKZSA-N 0.000 description 1
- ROHFNLRQFUQHCH-YFKPBYRVSA-N L-leucine Chemical compound CC(C)C[C@H](N)C(O)=O ROHFNLRQFUQHCH-YFKPBYRVSA-N 0.000 description 1
- KZSNJWFQEVHDMF-BYPYZUCNSA-N L-valine Chemical compound CC(C)[C@H](N)C(O)=O KZSNJWFQEVHDMF-BYPYZUCNSA-N 0.000 description 1
- 108010080643 L-xylulose reductase Proteins 0.000 description 1
- 102100029137 L-xylulose reductase Human genes 0.000 description 1
- 101150044775 LYS1 gene Proteins 0.000 description 1
- 240000001929 Lactobacillus brevis Species 0.000 description 1
- 235000013957 Lactobacillus brevis Nutrition 0.000 description 1
- 241000194036 Lactococcus Species 0.000 description 1
- 235000019687 Lamb Nutrition 0.000 description 1
- ROHFNLRQFUQHCH-UHFFFAOYSA-N Leucine Natural products CC(C)CC(N)C(O)=O ROHFNLRQFUQHCH-UHFFFAOYSA-N 0.000 description 1
- 101500023488 Lithobates catesbeianus GnRH-associated peptide 1 Proteins 0.000 description 1
- 241000555676 Malassezia Species 0.000 description 1
- 241000124008 Mammalia Species 0.000 description 1
- 102100029778 Melanoma inhibitory activity protein 2 Human genes 0.000 description 1
- 102000018697 Membrane Proteins Human genes 0.000 description 1
- 108010052285 Membrane Proteins Proteins 0.000 description 1
- 108010086428 NADH Dehydrogenase Proteins 0.000 description 1
- 102000006746 NADH Dehydrogenase Human genes 0.000 description 1
- 102100032199 NADH dehydrogenase [ubiquinone] 1 alpha subcomplex subunit 5 Human genes 0.000 description 1
- BOPGDPNILDQYTO-NNYOXOHSSA-L NADH(2-) Chemical compound C1=CCC(C(=O)N)=CN1[C@H]1[C@H](O)[C@H](O)[C@@H](COP([O-])(=O)OP([O-])(=O)OC[C@@H]2[C@H]([C@@H](O)[C@@H](O2)N2C3=NC=NC(N)=C3N=C2)O)O1 BOPGDPNILDQYTO-NNYOXOHSSA-L 0.000 description 1
- 101150082943 NAT1 gene Proteins 0.000 description 1
- 101150113561 NUP57 gene Proteins 0.000 description 1
- 101100073341 Oryza sativa subsp. japonica KAO gene Proteins 0.000 description 1
- 101150110652 PDC2 gene Proteins 0.000 description 1
- KJWZYMMLVHIVSU-IYCNHOCDSA-N PGK1 Chemical compound CCCCC[C@H](O)\C=C\[C@@H]1[C@@H](CCCCCCC(O)=O)C(=O)CC1=O KJWZYMMLVHIVSU-IYCNHOCDSA-N 0.000 description 1
- 101150093629 PYK1 gene Proteins 0.000 description 1
- 241000194105 Paenibacillus polymyxa Species 0.000 description 1
- 102000002508 Peptide Elongation Factors Human genes 0.000 description 1
- 108010068204 Peptide Elongation Factors Proteins 0.000 description 1
- 101150018379 Pfk1 gene Proteins 0.000 description 1
- 102100028251 Phosphoglycerate kinase 1 Human genes 0.000 description 1
- OAICVXFJPJFONN-UHFFFAOYSA-N Phosphorus Chemical compound [P] OAICVXFJPJFONN-UHFFFAOYSA-N 0.000 description 1
- 108091000080 Phosphotransferase Proteins 0.000 description 1
- 241000235379 Piromyces Species 0.000 description 1
- 206010035664 Pneumonia Diseases 0.000 description 1
- 206010035717 Pneumonia klebsiella Diseases 0.000 description 1
- 108020005115 Pyruvate Kinase Proteins 0.000 description 1
- 102000013009 Pyruvate Kinase Human genes 0.000 description 1
- 108700005075 Regulator Genes Proteins 0.000 description 1
- 108091006631 SLC13A4 Proteins 0.000 description 1
- 101100010928 Saccharolobus solfataricus (strain ATCC 35092 / DSM 1617 / JCM 11322 / P2) tuf gene Chemical group 0.000 description 1
- 241000235072 Saccharomyces bayanus Species 0.000 description 1
- 101100177143 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) HAA1 gene Proteins 0.000 description 1
- 101100451954 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) HXT1 gene Proteins 0.000 description 1
- 101100507949 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) HXT2 gene Proteins 0.000 description 1
- 101100507954 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) HXT5 gene Proteins 0.000 description 1
- 101100453262 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) JEN1 gene Proteins 0.000 description 1
- 101100082596 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) PDC5 gene Proteins 0.000 description 1
- 101100519200 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) PDC6 gene Proteins 0.000 description 1
- 101100174606 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) TDH2 gene Proteins 0.000 description 1
- 101100174613 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) TDH3 gene Proteins 0.000 description 1
- 101100045759 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) TFC1 gene Proteins 0.000 description 1
- 241000204893 Saccharomyces douglasii Species 0.000 description 1
- 241000235060 Scheffersomyces stipitis Species 0.000 description 1
- 241000235347 Schizosaccharomyces pombe Species 0.000 description 1
- 101100042410 Schizosaccharomyces pombe (strain 972 / ATCC 24843) sfc1 gene Proteins 0.000 description 1
- RDYSDCWZHHUGIB-UHFFFAOYSA-N Siamine Natural products OC1=CC(O)=C2C(=O)NC(C)=CC2=C1 RDYSDCWZHHUGIB-UHFFFAOYSA-N 0.000 description 1
- CDBYLPFSWZWCQE-UHFFFAOYSA-L Sodium Carbonate Chemical compound [Na+].[Na+].[O-]C([O-])=O CDBYLPFSWZWCQE-UHFFFAOYSA-L 0.000 description 1
- 102100033769 Sodium-coupled neutral amino acid transporter 3 Human genes 0.000 description 1
- 102100035209 Solute carrier family 13 member 4 Human genes 0.000 description 1
- 241000203644 Streptoalloteichus hindustanus Species 0.000 description 1
- 244000057717 Streptococcus lactis Species 0.000 description 1
- 235000014897 Streptococcus lactis Nutrition 0.000 description 1
- 101100029430 Streptomyces coelicolor (strain ATCC BAA-471 / A3(2) / M145) pfkA1 gene Proteins 0.000 description 1
- 101000666920 Streptomyces hygroscopicus subsp. limoneus Validoxylamine A 7'-phosphate phosphatase Proteins 0.000 description 1
- 241000187310 Streptomyces noursei Species 0.000 description 1
- 101150001810 TEAD1 gene Chemical group 0.000 description 1
- 101150010219 TEF2 gene Proteins 0.000 description 1
- 101150052008 TKL-1 gene Proteins 0.000 description 1
- 241000229115 Torulaspora globosa Species 0.000 description 1
- 102100029898 Transcriptional enhancer factor TEF-1 Human genes 0.000 description 1
- XSTXAVWGXDQKEL-UHFFFAOYSA-N Trichloroethylene Chemical group ClC=C(Cl)Cl XSTXAVWGXDQKEL-UHFFFAOYSA-N 0.000 description 1
- 241000499912 Trichoderma reesei Species 0.000 description 1
- KZSNJWFQEVHDMF-UHFFFAOYSA-N Valine Natural products CC(C)C(N)C(O)=O KZSNJWFQEVHDMF-UHFFFAOYSA-N 0.000 description 1
- 244000290333 Vanilla fragrans Species 0.000 description 1
- 235000009499 Vanilla fragrans Nutrition 0.000 description 1
- 235000012036 Vanilla tahitensis Nutrition 0.000 description 1
- 241000700605 Viruses Species 0.000 description 1
- 108700040099 Xylose isomerases Proteins 0.000 description 1
- 241000235013 Yarrowia Species 0.000 description 1
- 240000008042 Zea mays Species 0.000 description 1
- 235000005824 Zea mays ssp. parviglumis Nutrition 0.000 description 1
- 235000002017 Zea mays subsp mays Nutrition 0.000 description 1
- 108010084455 Zeocin Proteins 0.000 description 1
- 241000235017 Zygosaccharomyces Species 0.000 description 1
- NRAUADCLPJTGSF-ZPGVOIKOSA-N [(2r,3s,4r,5r,6r)-6-[[(3as,7r,7as)-7-hydroxy-4-oxo-1,3a,5,6,7,7a-hexahydroimidazo[4,5-c]pyridin-2-yl]amino]-5-[[(3s)-3,6-diaminohexanoyl]amino]-4-hydroxy-2-(hydroxymethyl)oxan-3-yl] carbamate Chemical compound NCCC[C@H](N)CC(=O)N[C@@H]1[C@@H](O)[C@H](OC(N)=O)[C@@H](CO)O[C@H]1\N=C/1N[C@H](C(=O)NC[C@H]2O)[C@@H]2N\1 NRAUADCLPJTGSF-ZPGVOIKOSA-N 0.000 description 1
- 241000222126 [Candida] glabrata Species 0.000 description 1
- 241000191335 [Candida] intermedia Species 0.000 description 1
- IKHGUXGNUITLKF-XPULMUKRSA-N acetaldehyde Chemical compound [14CH]([14CH3])=O IKHGUXGNUITLKF-XPULMUKRSA-N 0.000 description 1
- 150000003792 acetoin derivatives Chemical class 0.000 description 1
- 230000009471 action Effects 0.000 description 1
- 239000000654 additive Substances 0.000 description 1
- 235000013334 alcoholic beverage Nutrition 0.000 description 1
- 230000001476 alcoholic effect Effects 0.000 description 1
- 108090000637 alpha-Amylases Proteins 0.000 description 1
- 102000004139 alpha-Amylases Human genes 0.000 description 1
- RNBGYGVWRKECFJ-ZXXMMSQZSA-N alpha-D-fructofuranose 1,6-bisphosphate Chemical compound O[C@H]1[C@H](O)[C@](O)(COP(O)(O)=O)O[C@@H]1COP(O)(O)=O RNBGYGVWRKECFJ-ZXXMMSQZSA-N 0.000 description 1
- 229940024171 alpha-amylase Drugs 0.000 description 1
- 125000000539 amino acid group Chemical group 0.000 description 1
- 235000019270 ammonium chloride Nutrition 0.000 description 1
- 229910000148 ammonium phosphate Inorganic materials 0.000 description 1
- 235000019289 ammonium phosphates Nutrition 0.000 description 1
- 239000003242 anti bacterial agent Substances 0.000 description 1
- 101150035354 araA gene Proteins 0.000 description 1
- 229910052786 argon Inorganic materials 0.000 description 1
- 238000003556 assay Methods 0.000 description 1
- 235000015173 baked goods and baking mixes Nutrition 0.000 description 1
- 230000004888 barrier function Effects 0.000 description 1
- 230000003796 beauty Effects 0.000 description 1
- 230000009286 beneficial effect Effects 0.000 description 1
- GUBGYTABKSRVRQ-QUYVBRFLSA-N beta-maltose Chemical compound OC[C@H]1O[C@H](O[C@H]2[C@H](O)[C@@H](O)[C@H](O)O[C@@H]2CO)[C@H](O)[C@@H](O)[C@@H]1O GUBGYTABKSRVRQ-QUYVBRFLSA-N 0.000 description 1
- 230000004071 biological effect Effects 0.000 description 1
- 230000006696 biosynthetic metabolic pathway Effects 0.000 description 1
- 150000005693 branched-chain amino acids Chemical class 0.000 description 1
- OWBTYPJTUOEWEK-UHFFFAOYSA-N butane-2,3-diol Chemical compound CC(O)C(C)O OWBTYPJTUOEWEK-UHFFFAOYSA-N 0.000 description 1
- 108010036467 butanediol dehydrogenase Proteins 0.000 description 1
- 235000014121 butter Nutrition 0.000 description 1
- 208000032343 candida glabrata infection Diseases 0.000 description 1
- 235000013736 caramel Nutrition 0.000 description 1
- 239000004202 carbamide Substances 0.000 description 1
- 235000013877 carbamide Nutrition 0.000 description 1
- 230000025938 carbohydrate utilization Effects 0.000 description 1
- 239000011203 carbon fibre reinforced carbon Substances 0.000 description 1
- BVKZGUZCCUSVTD-UHFFFAOYSA-N carbonic acid Chemical compound OC(O)=O BVKZGUZCCUSVTD-UHFFFAOYSA-N 0.000 description 1
- 230000001925 catabolic effect Effects 0.000 description 1
- 239000003054 catalyst Substances 0.000 description 1
- 230000034303 cell budding Effects 0.000 description 1
- 238000004113 cell culture Methods 0.000 description 1
- 230000010261 cell growth Effects 0.000 description 1
- 230000004663 cell proliferation Effects 0.000 description 1
- 230000019522 cellular metabolic process Effects 0.000 description 1
- 238000001311 chemical methods and process Methods 0.000 description 1
- 238000012411 cloning technique Methods 0.000 description 1
- 150000001868 cobalt Chemical class 0.000 description 1
- 235000016213 coffee Nutrition 0.000 description 1
- 235000013353 coffee beverage Nutrition 0.000 description 1
- 239000008373 coffee flavor Substances 0.000 description 1
- 238000009833 condensation Methods 0.000 description 1
- 230000005494 condensation Effects 0.000 description 1
- 239000003636 conditioned culture medium Substances 0.000 description 1
- 235000009508 confectionery Nutrition 0.000 description 1
- 238000010276 construction Methods 0.000 description 1
- 238000010924 continuous production Methods 0.000 description 1
- 235000005822 corn Nutrition 0.000 description 1
- 239000006071 cream Substances 0.000 description 1
- 238000006114 decarboxylation reaction Methods 0.000 description 1
- 238000011161 development Methods 0.000 description 1
- MNNHAPBLZZVQHP-UHFFFAOYSA-N diammonium hydrogen phosphate Chemical compound [NH4+].[NH4+].OP([O-])([O-])=O MNNHAPBLZZVQHP-UHFFFAOYSA-N 0.000 description 1
- 229910001882 dioxygen Inorganic materials 0.000 description 1
- XPPKVPWEQAFLFU-UHFFFAOYSA-J diphosphate(4-) Chemical compound [O-]P([O-])(=O)OP([O-])([O-])=O XPPKVPWEQAFLFU-UHFFFAOYSA-J 0.000 description 1
- 235000011180 diphosphates Nutrition 0.000 description 1
- ZPWVASYFFYYZEW-UHFFFAOYSA-L dipotassium hydrogen phosphate Chemical compound [K+].[K+].OP([O-])([O-])=O ZPWVASYFFYYZEW-UHFFFAOYSA-L 0.000 description 1
- 229910000396 dipotassium phosphate Inorganic materials 0.000 description 1
- 235000019797 dipotassium phosphate Nutrition 0.000 description 1
- 150000002016 disaccharides Chemical class 0.000 description 1
- 230000002222 downregulating effect Effects 0.000 description 1
- 230000003828 downregulation Effects 0.000 description 1
- 230000008030 elimination Effects 0.000 description 1
- 238000003379 elimination reaction Methods 0.000 description 1
- 229940092559 enterobacter aerogenes Drugs 0.000 description 1
- 229940032049 enterococcus faecalis Drugs 0.000 description 1
- 238000003912 environmental pollution Methods 0.000 description 1
- 230000009483 enzymatic pathway Effects 0.000 description 1
- 238000011067 equilibration Methods 0.000 description 1
- 230000029142 excretion Effects 0.000 description 1
- 239000000284 extract Substances 0.000 description 1
- 238000012262 fermentative production Methods 0.000 description 1
- 235000013355 food flavoring agent Nutrition 0.000 description 1
- 238000009472 formulation Methods 0.000 description 1
- 239000012634 fragment Substances 0.000 description 1
- 239000003205 fragrance Substances 0.000 description 1
- 229940025237 fructose 1,6-diphosphate Drugs 0.000 description 1
- 239000008369 fruit flavor Substances 0.000 description 1
- 235000011852 gelatine desserts Nutrition 0.000 description 1
- 108091008053 gene clusters Proteins 0.000 description 1
- 238000012224 gene deletion Methods 0.000 description 1
- 238000010363 gene targeting Methods 0.000 description 1
- 235000021472 generally recognized as safe Nutrition 0.000 description 1
- 238000010353 genetic engineering Methods 0.000 description 1
- 150000004676 glycans Chemical class 0.000 description 1
- 102000006602 glyceraldehyde-3-phosphate dehydrogenase Human genes 0.000 description 1
- 108020004445 glyceraldehyde-3-phosphate dehydrogenase Proteins 0.000 description 1
- 239000007952 growth promoter Substances 0.000 description 1
- 239000001307 helium Substances 0.000 description 1
- 229910052734 helium Inorganic materials 0.000 description 1
- SWQJXJOGLNCZEY-UHFFFAOYSA-N helium atom Chemical compound [He] SWQJXJOGLNCZEY-UHFFFAOYSA-N 0.000 description 1
- 150000002402 hexoses Chemical class 0.000 description 1
- 238000004128 high performance liquid chromatography Methods 0.000 description 1
- 238000002744 homologous recombination Methods 0.000 description 1
- 230000006801 homologous recombination Effects 0.000 description 1
- 101150029559 hph gene Proteins 0.000 description 1
- 239000001257 hydrogen Substances 0.000 description 1
- 229910052739 hydrogen Inorganic materials 0.000 description 1
- 125000004435 hydrogen atom Chemical class [H]* 0.000 description 1
- 230000002209 hydrophobic effect Effects 0.000 description 1
- 230000006872 improvement Effects 0.000 description 1
- 230000006698 induction Effects 0.000 description 1
- 238000009776 industrial production Methods 0.000 description 1
- 229910052500 inorganic mineral Inorganic materials 0.000 description 1
- 238000002955 isolation Methods 0.000 description 1
- 229960000310 isoleucine Drugs 0.000 description 1
- AGPKZVBTJJNPAG-UHFFFAOYSA-N isoleucine Natural products CCC(C)C(N)C(O)=O AGPKZVBTJJNPAG-UHFFFAOYSA-N 0.000 description 1
- 239000002029 lignocellulosic biomass Substances 0.000 description 1
- 159000000003 magnesium salts Chemical class 0.000 description 1
- 238000012423 maintenance Methods 0.000 description 1
- 150000002696 manganese Chemical class 0.000 description 1
- 239000000463 material Substances 0.000 description 1
- 239000011159 matrix material Substances 0.000 description 1
- 235000013372 meat Nutrition 0.000 description 1
- 230000007246 mechanism Effects 0.000 description 1
- 239000012528 membrane Substances 0.000 description 1
- 108020004999 messenger RNA Proteins 0.000 description 1
- 229910052751 metal Inorganic materials 0.000 description 1
- 239000002184 metal Substances 0.000 description 1
- 230000007483 microbial process Effects 0.000 description 1
- 239000011707 mineral Substances 0.000 description 1
- 235000010755 mineral Nutrition 0.000 description 1
- 235000013379 molasses Nutrition 0.000 description 1
- 229910000402 monopotassium phosphate Inorganic materials 0.000 description 1
- 235000019796 monopotassium phosphate Nutrition 0.000 description 1
- 231100000062 no-observed-adverse-effect level Toxicity 0.000 description 1
- 235000019520 non-alcoholic beverage Nutrition 0.000 description 1
- TVMXDCGIABBOFY-UHFFFAOYSA-N octane Chemical compound CCCCCCCC TVMXDCGIABBOFY-UHFFFAOYSA-N 0.000 description 1
- 238000005457 optimization Methods 0.000 description 1
- 230000003204 osmotic effect Effects 0.000 description 1
- 230000001590 oxidative effect Effects 0.000 description 1
- 230000020477 pH reduction Effects 0.000 description 1
- 239000003208 petroleum Substances 0.000 description 1
- CWCMIVBLVUHDHK-ZSNHEYEWSA-N phleomycin D1 Chemical compound N([C@H](C(=O)N[C@H](C)[C@@H](O)[C@H](C)C(=O)N[C@@H]([C@H](O)C)C(=O)NCCC=1SC[C@@H](N=1)C=1SC=C(N=1)C(=O)NCCCCNC(N)=N)[C@@H](O[C@H]1[C@H]([C@@H](O)[C@H](O)[C@H](CO)O1)O[C@@H]1[C@H]([C@@H](OC(N)=O)[C@H](O)[C@@H](CO)O1)O)C=1N=CNC=1)C(=O)C1=NC([C@H](CC(N)=O)NC[C@H](N)C(N)=O)=NC(N)=C1C CWCMIVBLVUHDHK-ZSNHEYEWSA-N 0.000 description 1
- 229910052698 phosphorus Inorganic materials 0.000 description 1
- 239000011574 phosphorus Substances 0.000 description 1
- 102000020233 phosphotransferase Human genes 0.000 description 1
- 101150000475 pntAB gene Proteins 0.000 description 1
- 108091033319 polynucleotide Proteins 0.000 description 1
- 102000040430 polynucleotide Human genes 0.000 description 1
- 239000002157 polynucleotide Substances 0.000 description 1
- 229920001282 polysaccharide Polymers 0.000 description 1
- 239000005017 polysaccharide Substances 0.000 description 1
- GNSKLFRGEWLPPA-UHFFFAOYSA-M potassium dihydrogen phosphate Chemical compound [K+].OP(O)([O-])=O GNSKLFRGEWLPPA-UHFFFAOYSA-M 0.000 description 1
- 239000002243 precursor Substances 0.000 description 1
- 238000002360 preparation method Methods 0.000 description 1
- 238000012545 processing Methods 0.000 description 1
- 230000001737 promoting effect Effects 0.000 description 1
- 230000010076 replication Effects 0.000 description 1
- 108091008146 restriction endonucleases Proteins 0.000 description 1
- 230000000717 retained effect Effects 0.000 description 1
- 101150005492 rpe1 gene Proteins 0.000 description 1
- 229960002181 saccharomyces boulardii Drugs 0.000 description 1
- 239000000523 sample Substances 0.000 description 1
- 238000002864 sequence alignment Methods 0.000 description 1
- 238000012163 sequencing technique Methods 0.000 description 1
- 238000004904 shortening Methods 0.000 description 1
- 230000006641 stabilisation Effects 0.000 description 1
- 238000011105 stabilization Methods 0.000 description 1
- 230000003068 static effect Effects 0.000 description 1
- 101150033131 sthA gene Proteins 0.000 description 1
- 238000003756 stirring Methods 0.000 description 1
- 125000000185 sucrose group Chemical group 0.000 description 1
- 239000013589 supplement Substances 0.000 description 1
- 230000001629 suppression Effects 0.000 description 1
- 101150088047 tdh3 gene Proteins 0.000 description 1
- 101150109723 tef3 gene Proteins 0.000 description 1
- 239000011573 trace mineral Substances 0.000 description 1
- 235000013619 trace mineral Nutrition 0.000 description 1
- 108091006106 transcriptional activators Proteins 0.000 description 1
- 230000009466 transformation Effects 0.000 description 1
- 241001515965 unidentified phage Species 0.000 description 1
- 230000003827 upregulation Effects 0.000 description 1
- 239000004474 valine Substances 0.000 description 1
- 238000009834 vaporization Methods 0.000 description 1
- 230000008016 vaporization Effects 0.000 description 1
- 239000011782 vitamin Substances 0.000 description 1
- 235000013343 vitamin Nutrition 0.000 description 1
- 229940088594 vitamin Drugs 0.000 description 1
- 229930003231 vitamin Natural products 0.000 description 1
- 229940041603 vitamin k 3 Drugs 0.000 description 1
- 235000020234 walnut Nutrition 0.000 description 1
- 239000002912 waste gas Substances 0.000 description 1
- 101150011516 xlnD gene Proteins 0.000 description 1
- 239000007222 ypd medium Substances 0.000 description 1
- UZVNCLCLJHPHIF-NOJKMYKQSA-J zinc;(1e)-2-(ethylcarbamoylamino)-n-methoxy-2-oxoethanimidoyl cyanide;manganese(2+);n-[2-(sulfidocarbothioylamino)ethyl]carbamodithioate Chemical compound [Mn+2].[Zn+2].[S-]C(=S)NCCNC([S-])=S.[S-]C(=S)NCCNC([S-])=S.CCNC(=O)NC(=O)C(\C#N)=N\OC UZVNCLCLJHPHIF-NOJKMYKQSA-J 0.000 description 1
Images
Classifications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Y—ENZYMES
- C12Y106/00—Oxidoreductases acting on NADH or NADPH (1.6)
- C12Y106/03—Oxidoreductases acting on NADH or NADPH (1.6) with oxygen as acceptor (1.6.3)
- C12Y106/03001—NAD(P)H oxidase (1.6.3.1), i.e. NOX1
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/11—DNA or RNA fragments; Modified forms thereof; Non-coding nucleic acids having a biological activity
- C12N15/52—Genes encoding for enzymes or proenzymes
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/63—Introduction of foreign genetic material using vectors; Vectors; Use of hosts therefor; Regulation of expression
- C12N15/79—Vectors or expression systems specially adapted for eukaryotic hosts
- C12N15/80—Vectors or expression systems specially adapted for eukaryotic hosts for fungi
- C12N15/81—Vectors or expression systems specially adapted for eukaryotic hosts for fungi for yeasts
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N9/00—Enzymes; Proenzymes; Compositions thereof; Processes for preparing, activating, inhibiting, separating or purifying enzymes
- C12N9/0004—Oxidoreductases (1.)
- C12N9/0006—Oxidoreductases (1.) acting on CH-OH groups as donors (1.1)
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N9/00—Enzymes; Proenzymes; Compositions thereof; Processes for preparing, activating, inhibiting, separating or purifying enzymes
- C12N9/0004—Oxidoreductases (1.)
- C12N9/0012—Oxidoreductases (1.) acting on nitrogen containing compounds as donors (1.4, 1.5, 1.6, 1.7)
- C12N9/0036—Oxidoreductases (1.) acting on nitrogen containing compounds as donors (1.4, 1.5, 1.6, 1.7) acting on NADH or NADPH (1.6)
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N9/00—Enzymes; Proenzymes; Compositions thereof; Processes for preparing, activating, inhibiting, separating or purifying enzymes
- C12N9/10—Transferases (2.)
- C12N9/1022—Transferases (2.) transferring aldehyde or ketonic groups (2.2)
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N9/00—Enzymes; Proenzymes; Compositions thereof; Processes for preparing, activating, inhibiting, separating or purifying enzymes
- C12N9/88—Lyases (4.)
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12P—FERMENTATION OR ENZYME-USING PROCESSES TO SYNTHESISE A DESIRED CHEMICAL COMPOUND OR COMPOSITION OR TO SEPARATE OPTICAL ISOMERS FROM A RACEMIC MIXTURE
- C12P7/00—Preparation of oxygen-containing organic compounds
- C12P7/02—Preparation of oxygen-containing organic compounds containing a hydroxy group
- C12P7/04—Preparation of oxygen-containing organic compounds containing a hydroxy group acyclic
- C12P7/16—Butanols
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12P—FERMENTATION OR ENZYME-USING PROCESSES TO SYNTHESISE A DESIRED CHEMICAL COMPOUND OR COMPOSITION OR TO SEPARATE OPTICAL ISOMERS FROM A RACEMIC MIXTURE
- C12P7/00—Preparation of oxygen-containing organic compounds
- C12P7/02—Preparation of oxygen-containing organic compounds containing a hydroxy group
- C12P7/04—Preparation of oxygen-containing organic compounds containing a hydroxy group acyclic
- C12P7/18—Preparation of oxygen-containing organic compounds containing a hydroxy group acyclic polyhydric
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12P—FERMENTATION OR ENZYME-USING PROCESSES TO SYNTHESISE A DESIRED CHEMICAL COMPOUND OR COMPOSITION OR TO SEPARATE OPTICAL ISOMERS FROM A RACEMIC MIXTURE
- C12P7/00—Preparation of oxygen-containing organic compounds
- C12P7/24—Preparation of oxygen-containing organic compounds containing a carbonyl group
- C12P7/26—Ketones
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Y—ENZYMES
- C12Y202/00—Transferases transferring aldehyde or ketonic groups (2.2)
- C12Y202/01—Transketolases and transaldolases (2.2.1)
- C12Y202/01006—Acetolactate synthase (2.2.1.6)
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Y—ENZYMES
- C12Y401/00—Carbon-carbon lyases (4.1)
- C12Y401/01—Carboxy-lyases (4.1.1)
- C12Y401/01001—Pyruvate decarboxylase (4.1.1.1)
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Y—ENZYMES
- C12Y401/00—Carbon-carbon lyases (4.1)
- C12Y401/01—Carboxy-lyases (4.1.1)
- C12Y401/01005—Acetolactate decarboxylase (4.1.1.5)
-
- Y—GENERAL TAGGING OF NEW TECHNOLOGICAL DEVELOPMENTS; GENERAL TAGGING OF CROSS-SECTIONAL TECHNOLOGIES SPANNING OVER SEVERAL SECTIONS OF THE IPC; TECHNICAL SUBJECTS COVERED BY FORMER USPC CROSS-REFERENCE ART COLLECTIONS [XRACs] AND DIGESTS
- Y02—TECHNOLOGIES OR APPLICATIONS FOR MITIGATION OR ADAPTATION AGAINST CLIMATE CHANGE
- Y02E—REDUCTION OF GREENHOUSE GAS [GHG] EMISSIONS, RELATED TO ENERGY GENERATION, TRANSMISSION OR DISTRIBUTION
- Y02E50/00—Technologies for the production of fuel of non-fossil origin
- Y02E50/10—Biofuels, e.g. bio-diesel
Landscapes
- Chemical & Material Sciences (AREA)
- Life Sciences & Earth Sciences (AREA)
- Organic Chemistry (AREA)
- Health & Medical Sciences (AREA)
- Engineering & Computer Science (AREA)
- Genetics & Genomics (AREA)
- Zoology (AREA)
- Wood Science & Technology (AREA)
- Bioinformatics & Cheminformatics (AREA)
- General Engineering & Computer Science (AREA)
- Biochemistry (AREA)
- General Health & Medical Sciences (AREA)
- Biotechnology (AREA)
- Microbiology (AREA)
- Biomedical Technology (AREA)
- Molecular Biology (AREA)
- Medicinal Chemistry (AREA)
- Chemical Kinetics & Catalysis (AREA)
- General Chemical & Material Sciences (AREA)
- Mycology (AREA)
- Physics & Mathematics (AREA)
- Biophysics (AREA)
- Plant Pathology (AREA)
- Micro-Organisms Or Cultivation Processes Thereof (AREA)
- Preparation Of Compounds By Using Micro-Organisms (AREA)
- Enzymes And Modification Thereof (AREA)
Description
- アセト乳酸シンターゼ又はALSをコードする1つ又は複数の核酸、
- アセト乳酸デカルボキシラーゼ又はALDをコードする1つ又は複数の核酸、及び
- NADHオキシダーゼ(NOXE)をコードする1つ又は複数のコピーの核酸
が挿入されている。
(I)5'-[遺伝子1]x1-3'及び5'-[遺伝子2]x2-3'及び5'-[遺伝子3]x3-3'、
(II)5'-[遺伝子1]x1-[遺伝子2]x2-3'及び5'-[遺伝子3]x3-3'、
(III)5'-[遺伝子1]x1-[遺伝子2]x2-[遺伝子3]x3-3'、並びに
その組合せ、
(式中:
- 「遺伝子1」は、ALS、ALD又はNOXEを含む群から選択される核酸を意味し;
- 「遺伝子2」は、ALS、ALD又はNOXEを含む群から選択されるが、遺伝子1とは異なる核酸を意味し;
- 「遺伝子3」は、ALS、ALD又はNOXEを含む群から選択されるが、遺伝子1及び2とは異なる核酸を意味し;
- 「ALS」は、アセト乳酸シンターゼをコードする核酸であり;
- 「ALD」は、アセト乳酸デカルボキシラーゼをコードする核酸であり;
- 「NOXE」は、NADHオキシダーゼをコードする核酸であり;
- 「x1」、「x2」及び「x3」のそれぞれは、相互に独立に、0から50、好ましくは0から20の範囲の整数を表し、
但し、前記組換え酵母は、ALS、ALD及びNOXEのそれぞれをコードする少なくとも1つの核酸を含む)
を含む群から選択される1つ又は複数のDNA構築物を含んでいてもよい。
(IIa) 5'-[(prom5)y1-遺伝子1-term5]x5-[prom1-遺伝子1-term1]x1-[prom2-遺伝子2-(term2)z1]x2-3'及び5'-[(prom3)y2-遺伝子3-(term3)z2]x3-3'
(式中:
- 遺伝子1、遺伝子2、遺伝子3、「x1」、「x2」及び「x3」は、例えば、上記で規定したものであり;
- 「x5」は、0又は1に等しい整数を表し;
- 「y1」、「y2」、「z1」及び「z2」は、相互に独立に、0又は1に等しい整数を表し;
- 前記組換え酵母が少なくとも2つの式(IIa)のDNA構築物を含む場合、「x1」、「x2」、「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は同一であってもよく又は異なっていてもよく;
- 「prom 1」は、遺伝子1をコードする配列の発現を制御する制御配列であり;
- 「prom 2」は、遺伝子2をコードする配列の発現を制御する制御配列であり;
- 「prom 3」は、遺伝子3をコードする配列の発現を制御する制御配列であり;
- 「prom 5」は、遺伝子1の発現を制御する制御配列であり、前記prom 5はprom 1と同一又は異なり;
- 「term 1」は、遺伝子1をコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 2」は、遺伝子2をコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 3」は、遺伝子3をコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 5」は、遺伝子1の発現を終了させる転写ターミネーター配列であり、前記term 5はterm 1と同一又は異なる)
を有するDNA構築物を含んでいてもよい。
(IIb) 5'-[(prom5)y1-ALS-term5]x5-[prom1-ALS-term1]x1-[prom2-ALD-(term2)z1]x2-3'及び5'-[(prom3)y2-NOXE-(term3)z2]x3-3'
(式中:
- ALS、ALD、NOXE;「x1」、「x2」、「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は、例えば、上記で規定したものであり;
- 前記組換え酵母が少なくとも2つの式(IIb)のDNA構築物を含む場合、「x1」、「x2」、「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は同一であってもよく又は異なっていてもよく;
- 「prom 1」は、アセト乳酸シンターゼをコードする配列の発現を制御する制御配列であり;
- 「prom 2」は、アセト乳酸デカルボキシラーゼをコードする配列の発現を制御する制御配列であり;
- 「prom 3」は、NADHオキシダーゼをコードする配列の発現を制御する制御配列であり;
- 「prom 5」は、アセト乳酸シンターゼをコードする配列の発現を制御する制御配列であり、前記prom 5はprom 1と同一又は異なり;
- 「term 1」は、アセト乳酸シンターゼをコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 2」は、アセト乳酸デカルボキシラーゼをコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 3」は、NADHオキシダーゼをコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 5」は、アセト乳酸シンターゼをコードする配列の発現を終了させる転写ターミネーター配列であり、前記term 5はterm 1と同一又は異なる)
を有するDNA構築物を含んでいてもよい。
(IIc) 5'-[(prom5)y1-ALS-term5]x5-[prom1-ALS-term1]x1-[prom2-ALD-(term2)z1]x2-3'及び5'-[(prom3)y2-NOXE-(term3)z2]x6-3';並びに
(IId) 5'-[(prom5)y1-ALS-term5]x5-[prom1-ALS-term1]x1-[prom2-ALD-(term2)z1]x2-3'及び5'-[(prom3)y2-NOXE-(term3)z2]x7-3'
(式中:
- ALS、ALD、NOXE;「prom1」、「prom2」、「prom3」、「prom5」、「term1」、「term2」、「term3」及び「term5」;「x1」、「x2」及び「x3」;及び「x5」、「y1」、「y2」、「z1」及び「z2」は、例えば、上記で規定したものであり;
- 「x1」から「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は各式(IIc)及び(IId)について同一又は異なり;並びに
- 「x6」及び「x7」は、0から50、好ましくは0から20、好ましくは0から12、より詳細には2から5、好ましくは3から4の範囲、及び更に好ましくは(better still)3に等しい整数を表し、但し、「x6」及び「x7」のうちの1つは0を表す)
のDNA構築物を含んでいてもよい。
(a)適切な培養培地において本発明による組換え酵母を培養する工程;及び
(c)アセトインを回収する工程
を含む。
本明細書で使用される、用語「微生物」は、人工的に改変されていない酵母を指す。微生物「アクセプター」に組み込まれ、発現することになる外来の遺伝因子を供する場合、又は遺伝子構築若しくはタンパク質発現のためのツールとして使用される場合に、微生物は「ドナー」となりうる。本発明の微生物は、アセトインの生合成のための遺伝子を発現する酵母のうちから選ばれる。
上述のように、本発明は、減少したピルビン酸デカルボキシラーゼ活性を有する組換え酵母に関し、そのゲノム中には以下のものが挿入されている:
- アセト乳酸シンターゼ又はALSをコードする1つ又は複数の核酸、
- アセト乳酸デカルボキシラーゼ又はALDをコードする1つ又は複数の核酸、及び
- NADHオキシダーゼ(又はNOXE)をコードする1つ又は複数のコピーの核酸。
(I) 5'-[遺伝子1]x1-3'及び5'-[遺伝子2]x2-3'及び5'-[遺伝子3]x3-3'、
(II) 5'-[遺伝子1]x1-[遺伝子2]x2-3'及び5'-[遺伝子3]x3-3'、
(III) 5'-[遺伝子1]x1-[遺伝子2]x2-[遺伝子3]x3-3'、並びに
その組合せ、
(式中:
- 「遺伝子1」は、ALS、ALD又はNOXEを含む群から選択される核酸を意味し;
- 「遺伝子2」は、ALS、ALD又はNOXEを含む群から選択されるが、遺伝子1とは異なる核酸を意味し;
- 「遺伝子3」は、ALS、ALD又はNOXEを含む群から選択されるが、遺伝子1及び2とは異なる核酸を意味し;
- 「ALS」は、アセト乳酸シンターゼをコードする核酸であり;
- 「ALD」は、アセト乳酸デカルボキシラーゼをコードする核酸であり;
- 「NOXE」は、NADHオキシダーゼをコードする核酸であり;
- 「x1」、「x2」及び「x3」のそれぞれは、相互に独立に、0から50、好ましくは0から20の範囲の整数を表し、
但し、前記組換え酵母は、ALS、ALD及びNOXEのそれぞれをコードする少なくとも1つの核酸を含む)
を含む群から選択される1つ又は複数のDNA構築物を含んでいてもよい。
(I) 5'-[ALS]2-3'及び5'-[ALD]2-3'及び5'-[NOXE]3-3'
上記式(I)のDNA構築物を含む組換え酵母は、減少したピルビン酸デカルボキシラーゼ活性を有し、そのゲノム中に導入される以下の3つのDNA部分構築物(i)から(iii):
(i)相互に同一又は異なり、2つの核酸を含むDNA部分構築物であって、各核酸はALSをコードし、前記DNA部分構築物は前記組換え酵母のゲノムにおける第1の位置に導入される、DNA部分構築物;
(ii)相互に同一又は異なり、2つの核酸を含むDNA部分構築物であって、各核酸はALDをコードし、前記DNA部分構築物は前記組換え酵母のゲノムにおける第2の位置に導入され、その位置はALSをコードする核酸を含むDNA部分構築物が挿入されている位置とは別個である、DNA部分構築物;並びに
(iii)相互に同一又は異なり、3つの核酸を含むDNA部分構築物であって、各核酸はNOXEをコードし、前記DNA部分構築物は前記組換え酵母のゲノムにおける第3の位置に導入され、その位置は、それぞれ、ALSをコードする核酸を含むDNA部分構築物及びALDをコードする核酸を含むDNA部分構築物が挿入されている、第1及び第2の位置とは別個である、DNA部分構築物
を有する。
(II) 5'-[ALS]2-[ALD]2-3'及び5'-[NOXE]3-3'
上記式(II)のDNA構築物を含む組換え酵母は、減少したピルビン酸デカルボキシラーゼ活性を有し、以下の2つのDNA部分構築物(A)及び(B)が挿入されているゲノムを有する:
(A)第1のDNA部分構築物5'-[ALS]2-[ALD]2-3'であって、前記組換え酵母のゲノムにおける第1の位置に導入され、以下のもの:
(i)相互に同一又は異なり、各核酸がALSをコードする、2つの核酸;及び
(ii)相互に同一又は異なり、各核酸がALDをコードする、2つの核酸
を含む前記第1のDNA部分構築物;並びに
(B)第2のDNA部分構築物5'-[NOXE]3-3'であって、前記組換え酵母のゲノムにおける第2の位置に導入され、その位置が、第1のDNA部分構築物が挿入されている第1の位置から離れており、(iii)相互に同一又は異なり、各々がNOXEをコードする3つの核酸を含む、前記第2のDNA部分構築物。
(III) 5'-[ALS]2-[ALD]2-[NOXE]3-3'
上記式(III)のDNA構築物を含む組換え酵母は、減少したピルビン酸デカルボキシラーゼ活性を有し、前記組換え酵母のゲノム中の所望の位置に位置する1つのDNA構築物が挿入されているゲノムを有し、前記DNA構築物は以下のもの:
(i)相互に同一又は異なり、各核酸がALSをコードする、2つの核酸;
(ii)相互に同一又は異なり、各核酸がALDをコードする、2つの核酸;及び
(iii)相互に同一又は異なり、各核酸がNOXEをコードする、3つの核酸
を含む。
- 単一のDNA構築物内の1コピーのALSは、前記DNA構築物に含まれる別のコピーのALSと同一であってもよく又は前記DNA構築物に含有される全ての他のコピーのALSと同一であってもよく、或いは、代わりに前記1コピーのALSは前記DNA構築物に含有される互いのコピーのALSと別個であってもよい。
- 単一のDNA構築物内の1コピーのALDは、前記DNA構築物に含まれる別のコピーのALDと同一であってもよく又は前記DNA構築物に含有される全ての他のコピーのALDと同一であってもよく、或いは、代わりに前記1コピーのALDは前記DNA構築物に含有される互いのコピーのALDと別個であってもよい。
- 単一のDNA構築物内の1コピーのNOXEは、前記DNA構築物に含まれる別のコピーのNOXEと同一であってもよく又は前記DNA構築物に含有される全ての他のコピーのNOXEと同一であってもよく、或いは、代わりに前記1コピーのNOXEは前記DNA構築物に含有される互いのコピーのNOXEと別個であってもよい。
(III) 5'-[ALS]1-[ALD]1-[NOXE]1-3'、及び
(I) 5'-[ALS]0-3'及び5'-[ALD]0-3'及び5'-[NOXE]12-3'
生じた組換え酵母は、減少したピルビン酸デカルボキシラーゼ活性を有し、以下の2つのDNA部分構築物(A)及び(B)が挿入されているゲノムを有する:
(A)第1のDNA部分構築物5'-[ALS]1-[ALD]1-[NOXE]1-3'であって、前記組換え酵母のゲノムにおける第1の位置に導入され、以下のもの:
(i)ALSをコードする1つの核酸;
(ii)ALDをコードする1つの核酸;及び
(iii)NOXEをコードする1つの核酸
を含む前記第1のDNA部分構築物;
並びに
(B)第2のDNA部分構築物5'-[ALS]0-3'及び5'-[ALD]0-3'及び5'-[NOXE]12-3'であって、前記組換え酵母のゲノムにおける第2の位置に導入され、以下のもの:
(i)NOXEをコードする12の核酸
を含む前記第2のDNA部分構築物。
(III-1) 5'-[ALS]1-[ALD]1-[NOXE]1-3'、
(III-2) 5'-[ALS]1-[ALD]1-[NOXE]1-3'、
(I) 5'-[ALS]0-3'及び5'-[ALD]0-3'及び5'-[NOXE]12-3'
生じた組換え酵母は、減少したピルビン酸デカルボキシラーゼ活性を有し、以下の3つのDNA部分構築物(A)、(B)及び(C)が挿入されているゲノムを有する:
(A)第1のDNA部分構築物5'-[ALS]1-[ALD]1-[NOXE]1-3'であって、前記組換え酵母のゲノムにおける第1の位置に導入され、以下のもの:
(i)ALSをコードする1つの核酸;
(ii)ALDをコードする1つの核酸;及び
(iii)NOXEをコードする1つの核酸
を含む前記第1のDNA部分構築物;
(B)第2のDNA部分構築物5'-[ALS]1-[ALD]1-[NOXE]1-3'であって、前記組換え酵母のゲノムにおける第2の位置に導入され、以下のもの:
(i)ALSをコードする1つの核酸;
(ii)ALDをコードする1つの核酸;及び
(iii)NOXEをコードする1つの核酸
を含む前記第2のDNA部分構築物;
並びに
(C)第3のDNA部分構築物5'-[ALS]0-3'及び5'-[ALD]0-3'及び5'-[NOXE]12-3'であって、前記組換え酵母のゲノムにおける第3の位置に導入され、以下のもの:
(i)NOXEをコードする12の核酸
を含む前記第3のDNA部分構築物。
(II-1) 5'-[ALS]1-[ALD]1-3'及び5'-[NOXE]0-3'、
(II-2) 5'-[ALS]1-[ALD]1-3'及び5'-[NOXE]0-3'、
(I) 5'-[ALS]0-3'及び5'-[ALD]0-3'及び5'-[NOXE]12-3'
(A)第1のDNA部分構築物5'-[ALS]1-[ALD]1-3'及び5'-[NOXE]0-3'であって、前記組換え酵母のゲノムにおける第1の位置に導入され、以下のもの:
(i)ALSをコードする1つの核酸;及び
(ii)ALDをコードする1つの核酸
を含む前記第1のDNA部分構築物;
(B)第2のDNA部分構築物5'-[ALS]1-[ALD]1-3'及び5'-[NOXE]0-3'であって、前記組換え酵母のゲノムにおける第2の位置に導入され、以下のもの:
(i)ALSをコードする1つの核酸;及び
(ii)ALDをコードする1つの核酸
を含む前記第2のDNA部分構築物;
並びに
(C)第3のDNA部分構築物5'-[NOXE]12-3'であって、前記組換え酵母のゲノムにおける第3の位置に導入され、その位置が、第1のDNA部分構築物が挿入されている第1の位置から離れており、(iii)相互に同一又は異なり、各々がNOXEをコードする、12の核酸を含むDNA部分構築物。
(IIa) 5'-[(prom5)y1-遺伝子1-term5]x5-[prom1-遺伝子1-term1]x1-[prom2-遺伝子2-(term2)z1]x2-3'及び5'-[(prom3)y2-遺伝子3-(term3)z2]x3-3'
(式中:
- 遺伝子1、遺伝子2及び遺伝子3、「x1」、「x2」及び「x3」は、例えば、上記で規定したものであり;
- 「x5」は、0又は1に等しい整数を表し;
- 「y1」、「y2」、「z1」及び「z2」は、相互に独立に、0又は1に等しい整数を表し;
- 前記組換え酵母が式(IIa)の少なくとも2つのDNA構築物を含む場合、「x1」、「x2」、「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は同一であってもよい又は異なっていてもよい;
- 「prom 1」は、遺伝子1をコードする配列の発現を制御する制御配列であり;
- 「prom 2」は、遺伝子2をコードする配列の発現を制御する制御配列であり;
- 「prom 3」は、遺伝子3をコードする配列の発現を制御する制御配列であり;
- 「prom 5」は、遺伝子1の発現を制御する制御配列であり、前記prom 5はprom 1と同一又は異なり;
- 「term 1」は、遺伝子1をコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 2」は、遺伝子2をコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 3」は、遺伝子3をコードする配列の発現を終了させる転写ターミネーター配列であり;及び
- 「term 5」は、遺伝子1の発現を終了させる転写ターミネーター配列であり、前記term 5はterm 1と同一又は異なる)
を有するDNA構築物を含んでいてもよい。
・「x5」が1に等しい整数であり、「y1」が0に等しい整数を表す場合、考慮される遺伝子1が、考慮されるDNA構築物が挿入されている組換え酵母の遺伝子のプロモーターの制御下にあることを意味する;又は
・「x5」が1に等しい整数であり、「y1」が1に等しい整数を表す場合、考慮される遺伝子1が、プロモーター「prom5」の制御下にあることを意味する。これに関して、DNA構築物が挿入される、内因性遺伝子の、好ましくはpdc遺伝子のプロモーターの配列は、排除される又は少なくとも中断され、並びにその関連するコード領域の配列である。
・「y2」が0に等しい整数である場合、考慮される遺伝子3が、考慮されるDNA構築物が挿入されている組換え酵母の遺伝子のプロモーターの制御下にあることを意味する;又は
・「y2」が1に等しい整数である場合、考慮される遺伝子3が、プロモーター「prom3」の制御下にあることを意味する。これに関して、DNA構築物が挿入される、内因性遺伝子のプロモーターの配列は、排除される又は少なくとも中断される、並びにその関連するコード領域の配列である。
・「z2」が0に等しい整数である場合、考慮される遺伝子3が、考慮されるDNA構築物が挿入されている組換え酵母の遺伝子の転写ターミネーターに連結されることを意味する;又は
・「z2」が1に等しい整数である場合、考慮される遺伝子3が、転写ターミネーター「term3」に連結されることを意味する。これに関して、DNA構築物が挿入される、内因性遺伝子の転写ターミネーターの配列は、排除される又は少なくとも中断され、並びにその関連するコード領域の配列である。
(IIb) 5'-[(prom5)y1-ALS-term5]x5-[prom1-ALS-term1]x1-[prom2-ALD-(term2)z1]x2-3'及び5'-[(prom3)y2-NOXE-(term3)z2]x3-3'
(式中:
- ALS、ALD、NOXE、「x1」、「x2」、「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は、例えば、上記で規定したものであり;
- 前記組換え酵母が少なくとも2つの式(IIb)のDNA構築物を含む場合、「x1」、「x2」、「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は同一であってもよく又は異なっていてもよく;
- 「prom 1」は、アセト乳酸シンターゼをコードする配列の発現を制御する制御配列であり;
- 「prom 2」は、アセト乳酸デカルボキシラーゼをコードする配列の発現を制御する制御配列であり;
- 「prom 3」は、NADHオキシダーゼをコードする配列の発現を制御する制御配列であり;
- 「prom 5」は、アセト乳酸シンターゼをコードする配列の発現を制御する制御配列であり、前記prom 5はprom 1と同一又は異なり;
- 「term 1」は、アセト乳酸シンターゼをコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 2」は、アセト乳酸デカルボキシラーゼをコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 3」は、NADHオキシダーゼをコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term 5」は、アセト乳酸シンターゼをコードする配列の発現を終了させる転写ターミネーター配列であり、前記term 5はterm 1と同一又は異なる)。
(IIc) 5'-[(prom5)y1-ALS-term5]x5-[prom1-ALS-term1]x1-[prom2-ALD-(term2)z1]x2-3'及び5'-[(prom3)y2-NOXE-(term3)z2]x6-3';並びに
(IId) 5'-[(prom5)y1-ALS-term5]x5-[prom1-ALS-term1]x1-[prom2-ALD--(term2)z1]x2-3'及び5'-[(prom3)y2-NOXE-(term3)z2]x7-3';
(式中:
- ALS、ALD、NOXE、「prom1」、「prom2」、「prom3」、「prom5」、「term1」、「term2」、「term3」、「term5」、「x1」、「x2」、「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は、例えば、上記で規定したものであり;並びに
- 「x1」から「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は各式(IIc)及び(IId)について同一又は異なり;並びに
- 「x6」及び「x7」は、0から50、好ましくは0から20、好ましくは0から12、より詳細には2から5、好ましくは3から4の範囲、及び更に好ましくは3に等しい整数を表し、但し、「x6」及び「x7」のうちの1つは0を表す)。
・本発明の1つのDNA構築物に関して、「x1」、「x2」及び/若しくは「x3」は、2以上の整数を表し:
o遺伝子1、遺伝子2及び/若しくは遺伝子3のうちの関連する核酸についての各コピーは、同一であってもよく若しくは異なっていてもよく;並びに/又は
o遺伝子1、遺伝子2及び/若しくは遺伝子3のうちの関連する核酸についての各コピーについてのプロモーター及び/若しくはターミネーターは、同一であってもよく若しくは異なっていてもよく;
・組換え酵母が少なくとも2つのDNA構築物を含む場合、前記少なくとも2つのDNA構築物は、以下のことに関して、同一であってもよく又は異なっていてもよい:
(i)DNA構築物が式(I)から(III)を含む群のうちから選択される式により特徴付けられうる、それらの一般式;
(ii)「x1」から「x3」及び「x5」から「x7」、「y1」、「y2」、「z1」及び/若しくは「z2」の値;
(iii)同じ遺伝子に関するプロモーターの性質;
(iv)同じ遺伝子に関するターミネーターの性質;並びに/又は
(v)ALS、ALD及びNOXEが、特に以下Table 1(表1)に示されるように、異なる属に属する生物から由来しうる、同じ遺伝子それ自体の性質。
酵母における内因性ピルビン酸デカルボキシラーゼ活性は、ピルビン酸をアセトアルデヒドに変換し、これは次にエタノールに又はアセチル-CoAにアセテートを経て変換される。
アセト乳酸シンターゼ(ALS)酵素(アセトヒドロキシ酸シンターゼ(AHAS)、α-アセトヒドロキシ酸シンセターゼ、α-アセトヒドロキシ酸シンターゼ、α-アセト乳酸シンターゼ、α-アセト乳酸シンセターゼ、アセトヒドロキシ酸シンセターゼ、アセトヒドロキシ酸シンターゼ、アセト乳酸ピルビン酸リアーゼ(カルボキシル化)、アセト乳酸シンセターゼとしても知られている)は、分枝状鎖アミノ酸(バリン、ロイシン、及びイソロイシン)の合成における第1のステップを触媒するタンパク質である。
アセト乳酸デカルボキシラーゼ(ALD)酵素(α-アセト乳酸デカルボキシラーゼ、(S)-2-ヒドロキシ-2-メチル-3-オキソブタノエートカルボキシ-リアーゼ、(S)-2-ヒドロキシ-2-メチル-3-オキソブタノエートカルボキシ-リアーゼ[(R)-2-アセトイン-形成]又は(S)-2-ヒドロキシ-2-メチル-3-オキソブタノエートカルボキシ-リアーゼ[(3R)-3-ヒドロキシブタン-2-オン-形成]としても知られている)は、リアーゼのファミリー、具体化には炭素間結合を切断し、ブタノエート代謝及びc5-分枝二塩基酸代謝に参加するカルボキシリアーゼに属する。
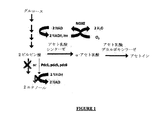
少なくとも1つのpdc遺伝子の活性の不活性化又は減少は、酵母におけるエタノール発酵経路を不活化又は減少させる。結果として、このことにより、ALS及びALDの発現によって解放されないアンバランスなレドックス状態が誘導される。実際、グルコースから2ピルビン酸への経路は、2NADH均等物を生成し、他方では、2ピルビン酸からアセトインへの転換はNADHからNAD+にリサイクルしない(図1を参照されたい)。
2NADH + 1/2O2 → 2NAD+ + H2O
明らかな理由のため、アセト乳酸シンターゼ、アセト乳酸デカルボキシラーゼ及びNADHオキシダーゼをコードする核酸のそれぞれは、同一又は異なる、プロモーターの制御下にある。
・アルコールデヒドロゲナーゼをコードする遺伝子からpADH1(ADH1遺伝子=配列番号32)、
・グリセルアルデヒド-3-リン酸デヒドロゲナーゼをコードする遺伝子からpTDH3(TDH3遺伝子=配列番号39)、
・翻訳伸長因子EF-1アルファをコードする遺伝子からpTEF2.Kl(TEF2遺伝子=配列番号30)、
・グリセリン酸ホスホムターゼをコードする遺伝子からpGPM1(GPM1遺伝子=配列番号33)、
・ピルビン酸デカルボキシラーゼをコードする遺伝子からpPDC1(PDC1遺伝子=配列番号35)、
・エノラーゼIIをコードする遺伝子からpENO2(ENO2遺伝子=配列番号29)、
・翻訳伸長因子eEF1Bのガンマサブユニットをコードする遺伝子からpTEF3(TEF3遺伝子=配列番号31)、
・フルクトース1,6-二リン酸エステルアルドラーゼIIをコードする遺伝子からpFBA1(FBA1遺伝子=配列番号34)、
・3-ホスホグリセリン酸キナーゼをコードする遺伝子からpPGK1(PGK1遺伝子=配列番号36)、
・ピルビン酸キナーゼをコードする遺伝子からpPYK1(PYK1遺伝子=配列番号49)、
・トリオースリン酸イソメラーゼをコードする遺伝子からpTPI1(TPI1遺伝子=配列番号50)、又は
・翻訳伸長因子EF-1アルファをコードする遺伝子からpTEF1(TEF1遺伝子=配列番号38)。
明らかな理由のため、アセト乳酸シンターゼ、アセト乳酸デカルボキシラーゼ及びNADHオキシダーゼをコードする核酸のそれぞれは、同一又は異なる、転写ターミネーター(本明細書において「ターミネーター」とも称されうる)に連結される。
・トリオースリン酸イソメラーゼをコードする遺伝子からtTPI1(TPI1遺伝子=配列番号44)、
・O-アセチルホモセリン-O-アセチルセリンスルフヒドリラーゼをコードする遺伝子からtMET25(Met25遺伝子=配列番号45)、
・アルコールデヒドロゲナーゼをコードする遺伝子からtADH1(ADH1遺伝子=配列番号43)、
・エノラーゼIIをコードする遺伝子からtENO2(ENO2遺伝子=配列番号46)、
・グリセルアルデヒド-3-リン酸デヒドロゲナーゼ、アイソザイム2をコードする遺伝子からtTDH2(TDH2遺伝子=配列番号40)、
・3-ホスホグリセリン酸キナーゼをコードする遺伝子からtPGK1(PGK1遺伝子=配列番号48)、
・tCYC1(=配列番号41)、
・tMET3(=配列番号47)、及び
・tTDH3(=配列番号42)、及び
・tDIT1(=配列番号43)。
一般に、酵母は、急速に増殖することができ、細菌と比較して高密度で培養することができ、産業上の設定において無菌的な環境を必要としない。更に、酵母細胞は、産物抽出及び精製のための非常に単純化されたプロセスで、細菌細胞と比較して、培養培地からより容易に分離することができる。
有利には、本発明において施行される酵素をコードする核酸は、ALS.Bs、ALS.Pp、ALD.Ll、ALD.Ea、NOXE.spn、NOXE.Ll及びそれらの混合物のうちから有利に選ばれる。
- 1つのpdc遺伝子、好ましくはpdc1遺伝子は、以下の式(IIe):
5'-[(prom5)y1-ALS.Bs-term5]x5-[prom1-ALS.Bs-term1]x1-[prom2-ALD.Ll-(term2)z1]x2-3' (IIe)
のDNA構築物の挿入によって破壊される、及び
- 上述の破壊されたpdc遺伝子と別個に、少なくとも他のpdc遺伝子、及び好ましくはpdc6遺伝子は、以下の式(IIf'):
5'-[(prom5)y1-ALS.Pp-term5]x5-[prom1-ALS.Pp-term1]x1-[prom2-ALD.Ea-(term2)z1]x2-3' (IIf')
のDNA構築物の挿入によって破壊される、
並びに、ここで、以下の式(IIf''):
5'-[(prom3)y2-NOXE.Ll-(term3)z2]x3-3' (IIf'')
のDNA構築物は、URA3遺伝子に挿入され、
式中:
- prom1、prom2、prom3、prom5、term1、term2、term3、term5、「y1」、「y2」、「z1」及び「z2」は、例えば、上記で規定され、ALS.Bs、ALS.Pp、ALD.Ll、ALD.Ea及びNOXE.Llは、例えば、以下のTable 1(表1)で規定され、
- 「x1」、「x2」及び「x3」のそれぞれは、相互に独立に、0から50、好ましくは0から20、好ましくは0から10、より詳細には0から3の範囲の、及び特に1に等しい整数を表し;
- 「x3」は、0から50、好ましくは0から20、好ましくは0から12、より詳細には2から5、好ましくは3から4の範囲、及び更に好ましくは3に等しい整数を表し、
但し、前記組換え酵母は、各ALS、ALD及びNOXEをコードする少なくとも1つの核酸を含み、但し、より詳細には式(IIe)及び(IIf')の各DNA構築物は、ALS及びALDをコードするそれぞれの少なくとも1つの核酸を含む。
- 「x1」から「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」;並びに/又は
- 考慮される遺伝子についての各コピーの核酸についてのプロモーター及び/又はターミネーターは、同一であってもよく又は異なっていてもよいことが特定される。
- 1つのpdc遺伝子、好ましくはpdc1遺伝子は、以下の式(IIg):
5'-[ALS.Bs-tTDH2]1-[pENO2-ALD.Ll-tCYC1]1-3' (IIg)
のDNA構築物の挿入によって破壊され、
- 上述の破壊されたpdc遺伝子と別個に、少なくとも他のpdc遺伝子、及び好ましくはpdc6遺伝子は、以下の式(IIh'):
5'-[pADH1-ALS.Pp-tDPI1]1-[pTDH3-ALD.Ea-tMET25]1-3' a (IIh')
のDNA構築物の挿入によって破壊され、
並びに、ここで、以下の式(IIh'')のDNA構築物:
5'-[pENO2-NOXE. Ll-tPGK1]12-3' (IIh'')
は、URA3遺伝子に挿入され、
ここで:
- 式(IIg)のDNA構築物の「ALS.Bs」遺伝子は、式(IIg)の前記DNA構築物が挿入される、pdc遺伝子のプロモーターの制御下にあり、
- pENO2、pADH1、pTDH3、tTDH2、tCYC1、tDPI1、tMET25及びtPGK1は、例えば、本記載において、並びに、より詳細には以下の配列表において規定され、
- ALS.Bs、ALS.Pp、ALD.Ll、ALD.Ea及びNOXE.Llは、例えば、以下のtable 1(表1)において、並びに、より詳細には以下の配列表において規定される。
糖の代替供給源、例えば、デンプンの直接的な使用は、外因性α-アミラーゼ及びグルコアミラーゼの酵母における過剰発現を更に必要とする(busckeら、biosource technology 2013)。
組換え微生物によるペントースの取込み輸送は、産業上のプロセスについての重要な課題であり、その理由は、C5糖が、加水分解されたリグノセルロース性バイオマスの主要な構成要素であるからである。多くの他のタイプの酵母の様な出芽酵母の天然の株は、発酵基質としてキシロース又はアラビノースのいずれも利用することができない(Hahn-Hagerdalら、2007;Jinら、2004)。興味深いことに、その株は、キシロースが天然の基質ではないとしても、その糖を取り込むことが可能である(Hamacherら、2002)。
キシロース及びアラビノース取込みを改善するために、組換えアセトイン産生株は、キシロース又はアラビノーストランスポーターをコードする異種遺伝子を発現するため改変されなければならない。例えば、カンジダインターメディア(Candida intermedia)、ピキアスティピティス(Pichia stipitis)及びシロイヌナズナ(Arabidopsis thaliana)のそれぞれからの遺伝子GXF1、SUT1及びAT5g59250は、酵母によるキシロース利用を改善するため過剰発現される(Runquistら、2010)。
酵母株は、キシロースが天然の基質ではないとしても、その糖を取込むことが可能である。キシロース同化作用についての遺伝子が出芽酵母中に存在するとしても、それらは有意な糖同化作用を可能にする十分なレベルで発現されない。したがって、遺伝的な改変は、ペントース糖の同化作用を改善するため必要である。キシロース又はアラビノースのキシリトールへの転換を可能にする全ての酵素が増強されること並びにキシリトールをキシルロースに及びキシルロースをキシルロース-5-リン酸に変換する酵素が必要である。キシロース及びアラビノース経路からの相同遺伝子は過剰発現されなければならないか又は細菌からの異種遺伝子は過剰発現されなければならないかのいずれかである。
1)P.スティピティスからのキシリトールデヒドロゲナーゼをコードするXYL2の過剰発現と関連させ、それぞれ出芽酵母及びP.スティピティスからのキシルロキナーゼをコードする遺伝子XKS1又はXYL3の過剰発現と組み合わせた、それぞれP.スティピティス及び出芽酵母のアルドラーゼレダクターゼをコードする遺伝子XYL1又はGRE3、
2)それぞれ出芽酵母及びP.スティピティスからのキシルロキナーゼをコードする遺伝子XKS1又はXYL3の過剰発現と関連させた細菌又はピロマイセス(Piromyces)からのキシロースイソメラーゼをコードする遺伝子xylA。
1)トリコデルマリーゼイ(Trichoderma reesei)からのL-アラビニトール4-ヒドロゲナーゼをコードするladl及びL-キシルロースレダクターゼをコードするIxrlと関連させ、P.スティピティスからのキシリトールデヒドロゲナーゼをコードするXYL2の過剰発現、並びに、加えて、それぞれ出芽酵母及びP.スティピティスからのキシルロキナーゼをコードする遺伝子XKS1又はXYL3の過剰発現と組み合わせた、それぞれP.スティピティス及び出芽酵母のアルドラーゼレダクターゼをコードする相同遺伝子XYL1又はGRE3、
2)細菌性アラビノースイソメラーゼ及びリブロースキナーゼをコードする異種遺伝子araA及びaraB。
これは、酵母株からの非酸化的ペントースリン酸経路に属する少なくとも1つの遺伝子;TALI、TKL1、RKL1及びRPE1を過剰発現によって行うことができる。
これは、酵母株において大腸菌のトランスヒドロゲナーゼ発現させることによって達成される。大腸菌からの遺伝子udhA及び/又はpntABは、産生株中で過剰発現される。
これは、グリセロール-3-リン酸デヒドロゲナーゼEC1.1.1.8.(GPDH)をコードするGPD1遺伝子の破壊によって行うことができる。
本発明はまた、アセトイン及び/又はその誘導体、特にメチルビニルケトン(MVK)の産生のための、例えば、上記で規定される、組換え酵母の使用に関する。
- 前に述べたような組換え微生物を用意する工程、炭素の供給源を含有する培養培地において組換え微生物を培養する工程、及び
- アセトインを回収する工程。
本発明の特定の態様によると、アセトインの発酵性産生は、培養培地からのアセトインの単離の工程を含む。培養培地からアセトインを回収する工程は、当業者にとってルーチン作業である。蒸留、ガスストリッピング、浸透気化法又は液体抽出を含むが、これらに限定されない、当該技術分野において周知される幾つかの技術によって達成されてもよい。当該分野における専門家は、どのようにして分離される物質の特徴に依存して各技術のパラメータに適合させるかについて知っている。
全ての以下の施行される組換え出芽酵母株を、標準株W303(Thomas及びRothstein (1989)、Cell. 56、619-630)から標準的な酵母分子遺伝学手順(Methods in yeast Genetics - A cold spring harbor laboratory course Manual (2000) by D. Burke、D. Dawson、T. Stearns CSHL Press)を用いて構築した。
- ade2、his3、leu2、trp1及びura3は、栄養要求性マーカー遺伝子である。
- 小文字は考慮される遺伝子が不活性であることを意味し、大文字は活性遺伝子を反映している。
- 遺伝子名に続く「::」:は、遺伝子が、続くものによって中断されることを意味する(一を超える遺伝子が挿入される場合に、それらは角型括弧[]中に注記される)。遺伝子の中断は、コード配列の全体的な欠失が付随するが、しかし、プロモーターは保存される。結果として、「::」が続く遺伝子は、不活性であり、小文字で注記される。特定されない場合に、挿入される遺伝子の転写は、破壊された遺伝子のプロモーターによって制御される。
- 「遺伝子.Kl」は、遺伝子が、クライベロマイセスラクティスに由来することを意味する。
- 所与の遺伝子の構成的な過剰発現を可能にする転写プロモーターは、文献(velculescuら、(1997) Cell 88、243-251)中に見出される。本明細書に使用されるプロモーターは、「p」と続くそれらの同族遺伝子名によって指定される。それらそれぞれの配列番号も、以下に記述される。
- 転写ターミネーターも、各遺伝子の後に配置される。不用な制御プロモーター及びターミネーター枠を回避するため、ある挿入される遺伝子は、同じオリジナル遺伝子から取得されなかった。本明細書に使用されるターミネーターは、「t」と続くそれらの同族遺伝子名によって指定される。それらそれぞれの配列番号も、以下に記述される。
ALS及びALD酵素は、個々に評価せず、アセトインの収率を通じて、ペア(ALS+ALD)で評価した。3つの外因性ALD及びALSを、それらの動力学的なパラメータに従って選び、ALS.Nt、ALS.Pp、ALS.Bs及びALD.Bb、ALD.Ll、ALD.Eaとした(上記を参照されたい)。
YA747: MAT-a、ade2、bdh1::TRP1.Kl、his3、leu2、pdc1::HIS5.Sp、pdc6::LEU2.Kl、trp1、ura3.
YA768: MAT-a、ade2、bdh1::TRP1.Kl、his3、leu2、pdc1:: [-ALS.Bs-tTPI1、pTDH3-ALD.Ea-tMET25、URA3.Kl]、pdc6::LEU2.Kl、trp1、ura3
NB:このケースでは、遺伝子「ALS.Bs」は、pdc1の天然プロモーター、すなわちプロモーターpPDC1の制御下にある。
YA769: MAT-a、ade2、bdh1::TRP1.Kl、his3、leu2、pdc1:: [-ALS.Nt-tTPI1、pTDH3-ALD.Ea-tMET25、URA3.Kl]、pdc6::LEU2.Kl、trp1、ura3
YA770: MAT-a、ade2、bdh1::TRP1.Kl、his3、leu2、pdc1::[-ALS.Pp-tTPI1、pTDH3-ALD.Ea-tMET25、URA3.Kl]、pdc6::LEU2.Kl、trp1、ura3
YA771: MAT-a、ade2、bdh1::TRP1.Kl、his3、leu2、pdc1::[-ALS.Nt-tTPI1、pTDH3-ALD.Bb-tMET25、URA3.Kl]、pdc6::LEU2.Kl、trp1、ura3
YA772: MAT-a、ade2、bdh1::TRP1.Kl、his3、leu2、pdc1::[- ALS.Nt-tTPI1、pTDH3-ALD.Ll-tMET25、URA3.Kl]、pdc6::LEU2.Kl、trp1、ura3
YA773: MAT-a、ade2、bdh1::TRP1.Kl、his3、leu2、pdc1::[-ALS.Pp-tTPI1、pTDH3-ALD.Ll-tMET25、URA3.Kl]、pdc6::LEU2.Kl、trp1、ura3
YA810: MAT-a、ade2、bdh1::TRP1.Kl、his3、leu2、pdc1::[-ALS.Bs-tTPI1、pTDH3-ALD.Bb-tMET25、URA3.Kl]、pdc6::LEU2.Kl、trp1、ura3
YA811: MAT-a、ade2、bdh1::TRP1.Kl、his3、leu2、pdc1::[-ALS.Pp-tTPI1、pTDH3-ALD.Bb-tMET25、URA3.Kl]、pdc6::LEU2.Kl、trp1、ura3
以下のTable 2(表2)は、上述の検査した株のアセトイン産生を示す。
YA1609による組換え酵母が、調製されている。
YA1609: MAT-a、his3、leu2、pdc1::[-ALS.Bs-tTDH2- pENO2-ALD.Ll- tCYC1、HIS5.Sp]、pdc6::[pADH1-ALS.Pp-tDPI1、pTDH3-ALD.Ea-tMET25、LEU2.Kl]、trp1、ura3::[pENO2-NOXE.Ll-tPGK1、URA3]x12
結果は、以下のTable 3(表3)に報告される。
環境:0.5l YPA、16%グルコース。
細胞培養の開始の16時間後、細胞を、16% w/wグルコースの最終濃度を含む培養培地中で8時間の期間インキュベートした。
撹拌:800rpm(2枚羽根)、1.9ms-1
温度:30℃
空気:0.15L/分(0.3vvm)
結果は、以下のTable 4(表4)に報告される。
更なる組換え酵母が、調製され、以下に記載される。
YA1573-4: MAT-a、his3、leu2、pdc1::[-ALS.Bs-tTDH2、pENO2-ALD.Ll-tCYC1、HIS5.Sp]、pdc6::[pADH1-ALS.Pp-tDPI1,pTDH3-ALD.Ea-tMET25,pTEF2-TRP1.Sc-tADH1,pGMP1-BDH.Sc-tENO2]、trp1、ura3::[pENO2-NOXE.Ll-tPGK1、URA3]x12
YA1609-4: MAT-a,his3、leu2、pdc1::[-ALS.Bs-tTDH2、pENO2-ALD.Ll-tCYC1、HIS5.Sp]、pdc6::[pADH1-ALS.Pp-tTPI1、pTDH3-ALD.Ea-tMET25、LEU2.Kl]、trp1、ura3::[pENO2-NOXE.Ll-tPGK1、URA3]x12
YA1661-2: MAT-a、his3、leu2、pdc1::[-ALS.Bs-tTDH2、pENO2-ALD.Ll-tCYC1、HIS5.Sp]、pdc6::[pADH1-ALS.Pp-tTPI1、pTDH3-ALD.Ea-tMET25、pENO2-NOXE.Spn-tPGK1]、trp1、ura3::[pENO2-NOXE.Ll-tPGK1、URA3]x12.
結果は、以下のTable 5(表5)に報告される。
以下の内因性bdh1、bdh2、adh1、adh3及び/又はadh4遺伝子のうち少なくとも1つの遺伝子が、不活化されてもよい。幾つかの株において、栄養要求性マーカーを再導入して、それらを原栄養体とした。それらは、全てYA1660と比べ同じプロモーター及びターミネーターを有する:
YA1660-2、YA1660-3、YA1660-4、及びYA1711-16C: MAT-a、his3、leu2、pdc1::[-ALS.Bs-tTDH2、pENO2-ALD.Ll-tCYC1、HIS5.Sp]、pdc6::[pADH1-ALS.Pp-tTPI1、pTDH3-ALD.Ea-tMET25、pENO2-NOXE.Spn-tPGK1、LEU2.Kl]、trp1、ura3::[pENO2-NOXE.Ll-tPGK1、URA3]x12.
YA1711-45c : Mat-α、his3、leu2、pdc1::[-ALS.Bs-tTDH2、pENO2-ALD.Ll-tCYC1、HIS5.Sp]、pdc6::[pADH1-ALS.Pp-tTPI1、pTDH3-ALD.Ea-tMET25、pENO2-NOXE.Spn-tPGK1、LEU2.Kl]、trp1、ura3::[pENO2-NOXE.Ll-tPGK1、URA3]x12
YA1711-13A、YA1711-16B: Mat-a、bdh1::LEU2.Kl、bdh2::HIS5.Sp、his3、leu2、pdc1::[ALS.Bs-ALD.Ll-HIS5.Sp]、pdc6::[ALS.Pp-ALD.Ea-NOXE.Spn-LEU2.Kl]、trp1、ura3::[NOXE.Ll-URA3]x12
YA1711-19A及びYA1711-46A: Mat-α、bdh1::LEU2.Kl、bdh2::HIS5.Sp、his3、leu2、pdc1::[ALS.Bs-ALD.Ll-HIS5.Sp]、pdc6::[ALS.Pp-ALD.Ea-NOXE.Spn-LEU2.Kl]、trp1、ura3::[NOXE.Ll-URA3]x12
YA1822-1及びYA1822-2: Mat-α、bdh1::LEU2.Kl、bdh2::HIS5.Sp、his3、leu2、pdc1::[ALS.Bs-ALD.Ll-HIS5.Sp]、pdc6::[ALS.Pp-ALD.Ea-NOXE.Spn-LEU2.Kl]、trp1::TRP1、ura3::[NOXE.Ll-URA3]x12
YA 1870-10A: Mat-a、adh3::TRP1.Kl、bdh1::LEU2.Kl、bdh2::HIS5.Sp、his3、leu2、pdc1::[ALS.Bs-ALD.Ll-HIS5.Sp]、pdc6::[ALS.Pp-ALD.Ea-NOXE.Spn-LEU2.Kl]、trp1、ura3::[NOXE.Ll-URA3]x12
YA 1870-11B: Mat-α、adh3::TRP1.Kl、bdh1::LEU2.Kl、bdh2::HIS5.Sp、his3、leu2、pdc1::[ALS.Bs-ALD.Ll-HIS5.Sp]、pdc6::[ALS.Pp-ALD.Ea-NOXE.Spn-LEU2.Kl]、trp1、ura3::[NOXE.Ll-URA3]x12
YA1870-10B: Mat-α、adh1::TRP1.Kl、bdh1::LEU2.Kl、bdh2::HIS5.Sp、his3、leu2、pdc1::[ALS.Bs-ALD.Ll-HIS5.Sp]、pdc6::[ALS.Pp-ALD.Ea-NOXE.Spn-LEU2.Kl]、trp1、ura3::[NOXE.Ll-URA3]x12
YA1870-11A: Mat-α、adh1::TRP1.Kl、bdh1::LEU2.Kl、bdh2::HIS5.Sp、his3、leu2、pdc1::[ALS.Bs-ALD.Ll-HIS5.Sp]、pdc6::[ALS.Pp-ALD.Ea-NOXE.Spn-LEU2.Kl]、trp1、ura3::[NOXE.Ll-URA3]x12
YA1870-2A及びYA1870-3D: Mat-a、adh1::TRP1.Kl、adh3::TRP1.Kl、bdh1::LEU2.Kl、bdh2::HIS5.Sp、his3、leu2、pdc1::[ALS.Bs-ALD.Ll-HIS5.Sp-loxP]、pdc6::[ALS.Pp-ALD.Ea-NOXE.Spn-LEU2.Kl-loxP]、trp1、ura3::[NOXE.Ll-URA3]x12
株YA1711-19Aを、3l発酵槽中、酵母抽出物2%、スクロース10%中で、0から24時間増殖させ、次に600gのグルコースをゆっくりと添加した(30g/lで20時間)。
Claims (15)
- 対応する非組換え酵母と比較して減少したピルビン酸デカルボキシラーゼ活性を有する、Saccharomyces cerevisiae(サッカロマイセス・セレビシエ)種に属する組換え酵母であって、そのゲノム中に:
- アセト乳酸シンターゼ(ALS)をコードする1つ又は複数の核酸、
- アセト乳酸デカルボキシラーゼ(ALD)をコードする1つ又は複数の核酸、並びに、
- 核酸配列の配列番号13又は15を有する核酸配列を有する、NADHオキシダーゼ(NOXE)をコードする1つ又は複数のコピーの核酸
が挿入されている組換え酵母。 - 以下の式を含む群から選択される1つ又は複数のDNA構築物を含む、請求項1に記載の組換え酵母:
(I) 5'-[遺伝子1]x1-3'及び5'-[遺伝子2]x2-3'及び5'-[遺伝子3]x3-3'、
(II) 5'-[遺伝子1]x1-[遺伝子2]x2-3'及び5'-[遺伝子3]x3-3'、
(III) 5'-[遺伝子1]x1-[遺伝子2]x2-[遺伝子3]x3-3'、並びに
その組合せ、
(式中:
- 「遺伝子1」は、ALS、ALD又はNOXEを含む群から選択される核酸を意味し;
- 「遺伝子2」は、ALS、ALD又はNOXEを含む群から選択されるが、遺伝子1とは異なる核酸を意味し;
- 「遺伝子3」は、ALS、ALD又はNOXEを含む群から選択されるが、遺伝子1及び2とは異なる核酸を意味し;
- 「ALS」は、アセト乳酸シンターゼをコードする核酸であり;
- 「ALD」は、アセト乳酸デカルボキシラーゼをコードする核酸であり;
- 「NOXE」は、NADHオキシダーゼをコードする核酸であり;
- 「x1」、「x2」及び「x3」のそれぞれは、相互に独立に、0から50の範囲の整数を表し、
但し、前記組換え酵母は、ALS、ALD及びNOXEのそれぞれをコードする少なくとも1つの核酸を含む)。 - 少なくとも1つの式(II)のDNA構築物を含み、「遺伝子3」がNADHオキシダーゼをコードする核酸を意味する、請求項2に記載の組換え酵母。
- 同一又は異なる、少なくとも1つの式(IIa)のDNA構築物を含み、各式(IIa)が以下の式を有する、請求項2に記載の組換え酵母:
(IIa) 5'-[(prom5)y1-遺伝子1-term5]x5-[prom1-遺伝子1-term1]x1-[prom2-遺伝子2-(term2)z1]x2-3'及び5'-[(prom3)y2-遺伝子3-(term3)z2]x3-3'
(式中:
- 遺伝子1、遺伝子2及び遺伝子3は、請求項2又は3に規定したものであり、「x1」、「x2」及び「x3」は、請求項2に規定したものであり;
- 「x5」は、0又は1に等しい整数を表し;
- 「y1」、「y2」、「z1」及び「z2」は、相互に独立に、0又は1に等しい整数を表し;
- 前記組換え酵母が少なくとも2つの式(IIa)のDNA構築物を含む場合、「x1」、「x2」、「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は同一であってもよく又は異なっていてもよく;
- 「prom1」は、遺伝子1をコードする配列の発現を制御する制御配列であり;
- 「prom2」は、遺伝子2をコードする配列の発現を制御する制御配列であり;
- 「prom3」は、遺伝子3をコードする配列の発現を制御する制御配列であり;
- 「prom5」は、遺伝子1の発現を制御する制御配列であり、前記prom5はprom1と同一又は異なり;
- 「term1」は、遺伝子1をコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term2」は、遺伝子2をコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term3」は、遺伝子3をコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term5」は、遺伝子1の発現を終了させる転写ターミネーター配列であり、前記term5はterm1と同一又は異なる)。 - 同一又は異なる、少なくとも1つの式(IIb)のDNA構築物を含み、各式(IIb)が以下の式を有する、請求項2に記載の組換え酵母:
(IIb) 5'-[(prom5)y1-ALS-term5]x5-[prom1-ALS-term1]x1-[prom2-ALD-(term2)z1]x2-3'及び5'-[(prom3)y2-NOXE-(term3)z2]x3-3'
(式中:
- ALS、ALD及びNOXEは、請求項1に規定したものであり;「x1」、「x2」及び「x3」は、請求項2に規定したものであり;「x5」及び「y1」、「y2」、「z1」及び「z2」は、請求項4に規定したものであり;
- 前記組換え酵母が少なくとも2つの式(IIb)のDNA構築物を含む場合、「x1」、「x2」、「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は同一であってもよく又は異なっていてもよく;
- 「prom1」は、アセト乳酸シンターゼをコードする配列の発現を制御する制御配列であり;
- 「prom2」は、アセト乳酸デカルボキシラーゼをコードする配列の発現を制御する制御配列であり;
- 「prom3」は、NADHオキシダーゼをコードする配列の発現を制御する制御配列であり;
- 「prom5」は、アセト乳酸シンターゼをコードする配列の発現を制御する制御配列であり、前記prom5はprom1と同一又は異なり;
- 「term1」は、アセト乳酸シンターゼをコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term2」は、アセト乳酸デカルボキシラーゼをコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term3」は、NADHオキシダーゼをコードする配列の発現を終了させる転写ターミネーター配列であり;
- 「term5」は、アセト乳酸シンターゼをコードする配列の発現を終了させる転写ターミネーター配列であり、前記term5はterm1と同一又は異なる)。 - 少なくとも2つの、式(II)、請求項4に規定される式(IIa)、又は、請求項5に規定される式(IIb)のDNA構築物を含み、但し、NOXEの核酸の全てのコピーは、少なくとも2つの式(II)、(IIa)又は(IIb)のDNA構築物の1つに位置する、請求項2に記載の組換え酵母。
- 少なくとも2つの、以下の式(IIc)及び(IId)のDNA構築物を含む、請求項2に記載の組換え酵母:
(IIc) 5'-[(prom5)y1-ALS-term5]x5-[prom1-ALS-term1]x1-[prom2-ALD-(term2)z1]x2-3'及び5'-[(prom3)y2-NOXE-(term3)z2]x6-3';並びに
(IId) 5'-[(prom5)y1-ALS-term5]x5-[prom1-ALS-term1]x1-[prom2-ALD-(term2)z1]x2-3'及び5'-[(prom3)y2-NOXE-(term3)z2]x7-3';
(式中:
- ALS、ALD及びNOXEは、請求項1に規定したものであり;「prom1」、「prom2」、「prom3」、「prom5」、「term1」、「term2」、「term3」及び「term5」は、請求項4から5のいずれか一項に規定したものであり;「x1」、及び、「x2」は、請求項2に規定したものであり;「x5」、「y1」、「y2」、「z1」及び「z2」は、請求項4に規定したものであり;
- 「x1」から「x3」、「x5」、「y1」、「y2」、「z1」及び「z2」は各式(IIc)及び(IId)について同一又は異なり;並びに
- 「x6」及び「x7」は、0から50の範囲の整数を表し、但し、「x6」及び「x7」のうちの1つは0を表す)。 - アセト乳酸シンターゼ(ALS)をコードする核酸は、核酸配列の配列番号1、3及び5からなる群から選択される核酸である、請求項1に記載の組換え酵母。
- アセト乳酸デカルボキシラーゼ(ALD)をコードする核酸は、核酸配列の配列番号7、9及び11からなる群から選択される核酸である、請求項1に記載の組換え酵母。
- ピルビン酸デカルボキシラーゼ活性は、少なくとも1つのpdc遺伝子の破壊によって減少される、請求項1に記載の組換え酵母。
- ピルビン酸デカルボキシラーゼ活性は、請求項2に規定される式(I)から(III)を含む群から選択される少なくとも1つのDNA構築物の挿入によって減少される、請求項10に記載の組換え酵母。
- 少なくともNOXE遺伝子を含む式(I)から(III)を含む群から選択されるDNA構築物は、前記組換え酵母の内因性URA3遺伝子に挿入される、請求項2に記載の組換え酵母。
- アセトイン又はメチルビニルケトンの産生のための、請求項1に記載の組換え酵母の使用。
- (a)請求項1に記載される組換え酵母を適切な培養培地において培養する工程;及び
(c)アセトインを回収する工程
を含む、アセトインを産生する方法。 - 前記培養培地は炭素源を含む、請求項14に記載の方法。
Applications Claiming Priority (3)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| EP14306205 | 2014-07-25 | ||
| EP14306205.7 | 2014-07-25 | ||
| PCT/EP2015/066927 WO2016012561A1 (en) | 2014-07-25 | 2015-07-23 | Method for producing acetoin |
Related Child Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2020136738A Division JP2020195384A (ja) | 2014-07-25 | 2020-08-13 | アセトインを産生する方法 |
Publications (2)
| Publication Number | Publication Date |
|---|---|
| JP2017525388A JP2017525388A (ja) | 2017-09-07 |
| JP6847036B2 true JP6847036B2 (ja) | 2021-03-24 |
Family
ID=51263347
Family Applications (2)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2017524104A Active JP6847036B2 (ja) | 2014-07-25 | 2015-07-23 | アセトインを産生する方法 |
| JP2020136738A Pending JP2020195384A (ja) | 2014-07-25 | 2020-08-13 | アセトインを産生する方法 |
Family Applications After (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2020136738A Pending JP2020195384A (ja) | 2014-07-25 | 2020-08-13 | アセトインを産生する方法 |
Country Status (11)
| Country | Link |
|---|---|
| US (1) | US10301655B2 (ja) |
| EP (1) | EP3172313A1 (ja) |
| JP (2) | JP6847036B2 (ja) |
| KR (1) | KR102281701B1 (ja) |
| CN (1) | CN106715679B (ja) |
| AU (1) | AU2015293864B2 (ja) |
| CA (1) | CA2956184C (ja) |
| IL (1) | IL250099B (ja) |
| NZ (1) | NZ728287A (ja) |
| RU (1) | RU2686614C2 (ja) |
| WO (1) | WO2016012561A1 (ja) |
Families Citing this family (10)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| CN106967741B (zh) * | 2017-04-03 | 2020-02-21 | 天津大学 | 一种体外酶反应生产l(+)-乙偶姻的方法 |
| CN107177620B (zh) * | 2017-06-28 | 2020-12-18 | 南宁中诺生物工程有限责任公司 | 一种利用廉价原料生产四甲基吡嗪的方法 |
| EP3428282A1 (en) * | 2017-07-11 | 2019-01-16 | Alderys | Ectoine-producing yeast |
| CN110914434A (zh) * | 2017-07-11 | 2020-03-24 | 安迪苏法国联合股份有限公司 | 苏氨酸生产酵母 |
| CN107955805B (zh) * | 2017-12-13 | 2020-03-06 | 江南大学 | 一种稳定性提高的nadh氧化酶及其在乙偶姻生产中的应用 |
| WO2019124782A2 (ko) * | 2017-12-20 | 2019-06-27 | 건국대학교 산학협력단 | 에탄올에서 아세토인, 부탄디올 또는 부탄올의 생산방법 |
| US11441142B2 (en) | 2017-12-20 | 2022-09-13 | Konkuk University Industrial Cooperation Corporation | FLS variant having increased activity |
| CN109370958A (zh) * | 2018-12-12 | 2019-02-22 | 佛山市海天(高明)调味食品有限公司 | 一株增加酱油中3-羟基-2-丁酮含量的植物乳杆菌及其应用 |
| CN110257442A (zh) * | 2019-06-03 | 2019-09-20 | 苏州凯祥生物科技有限公司 | 一种含混合糖浆香料的特异糖原培养基、制备方法及应用 |
| CN116287028A (zh) * | 2023-03-10 | 2023-06-23 | 天津大学 | 一种生物酶法利用甲醛合成乙偶姻的方法 |
Family Cites Families (6)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| SU777059A1 (ru) * | 1978-12-06 | 1980-11-07 | Институт Биохимии И Физиологии Микроорганизмов Ан Ссср | Способ выделени ацетоина |
| FR2887258B1 (fr) * | 2005-06-17 | 2007-09-21 | Agronomique Inst Nat Rech | Souches de levures saccharomyces transformees presentant une production d'ethanol reduite par fermentation |
| JP5437631B2 (ja) * | 2005-07-01 | 2014-03-12 | ザ ユニバーシティー オブ フロリダ リサーチ ファンデーション インク | エタノール産生のための組み換えホスト細胞及び培地 |
| FR2916000B1 (fr) * | 2007-05-07 | 2013-07-05 | Lallemand Sas | Moyens pour reduire l'accumulation d'acetoine dans des milieux de fermentation alcoolique |
| US9260708B2 (en) | 2009-09-29 | 2016-02-16 | Butamax Advanced Biofuels Llc | Yeast production host cells |
| US20140342419A1 (en) * | 2011-11-21 | 2014-11-20 | Metabolic Explorer | Microorganism strains for the production of 2,3-butanediol |
-
2015
- 2015-07-23 AU AU2015293864A patent/AU2015293864B2/en active Active
- 2015-07-23 WO PCT/EP2015/066927 patent/WO2016012561A1/en active Application Filing
- 2015-07-23 CA CA2956184A patent/CA2956184C/en active Active
- 2015-07-23 KR KR1020177005199A patent/KR102281701B1/ko active IP Right Grant
- 2015-07-23 JP JP2017524104A patent/JP6847036B2/ja active Active
- 2015-07-23 CN CN201580052256.XA patent/CN106715679B/zh active Active
- 2015-07-23 US US15/327,207 patent/US10301655B2/en active Active
- 2015-07-23 RU RU2017101673A patent/RU2686614C2/ru active
- 2015-07-23 NZ NZ728287A patent/NZ728287A/en unknown
- 2015-07-23 EP EP15749744.7A patent/EP3172313A1/en active Pending
-
2017
- 2017-01-15 IL IL250099A patent/IL250099B/en unknown
-
2020
- 2020-08-13 JP JP2020136738A patent/JP2020195384A/ja active Pending
Also Published As
| Publication number | Publication date |
|---|---|
| JP2017525388A (ja) | 2017-09-07 |
| WO2016012561A1 (en) | 2016-01-28 |
| CN106715679B (zh) | 2021-07-02 |
| CN106715679A (zh) | 2017-05-24 |
| IL250099A0 (en) | 2017-08-31 |
| IL250099B (en) | 2021-12-01 |
| KR102281701B1 (ko) | 2021-07-23 |
| CA2956184C (en) | 2021-10-19 |
| US20170159081A1 (en) | 2017-06-08 |
| RU2017101673A (ru) | 2018-08-30 |
| AU2015293864B2 (en) | 2019-07-11 |
| BR112017001542A2 (pt) | 2018-01-30 |
| KR20170041768A (ko) | 2017-04-17 |
| RU2017101673A3 (ja) | 2018-12-06 |
| CA2956184A1 (en) | 2016-01-28 |
| AU2015293864A1 (en) | 2017-02-02 |
| US10301655B2 (en) | 2019-05-28 |
| EP3172313A1 (en) | 2017-05-31 |
| RU2686614C2 (ru) | 2019-04-29 |
| NZ728287A (en) | 2019-01-25 |
| JP2020195384A (ja) | 2020-12-10 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| JP6847036B2 (ja) | アセトインを産生する方法 | |
| EP2783007B9 (en) | Microorganism strains for the production of 2,3-butanediol | |
| CN105121637B (zh) | 酿酒酵母中替代甘油形成的消耗电子的乙醇生产途径 | |
| US9994877B2 (en) | Yeast cell having acid tolerance, method of preparing yeast cell and use thereof | |
| JP6942878B2 (ja) | エクトイン産生酵母 | |
| JP2011507532A (ja) | 高収率でイソブタノールを産生する酵母生物 | |
| JP2014506478A (ja) | 組換え微生物およびそれらの使用 | |
| KR101616171B1 (ko) | 유기산 제조에서의 모나스쿠스의 용도 | |
| WO2018172328A1 (en) | Improved glycerol free ethanol production | |
| US20180030482A1 (en) | Use of acetaldehyde in the fermentative production of ethanol | |
| US10619174B2 (en) | Microorganism strains for the production of 2.3-butanediol | |
| EP3762499A1 (en) | Reduction in acetate production by yeast over-expressing pab1 | |
| WO2015141705A1 (ja) | 耐酸耐塩性付与方法と耐酸耐塩性酵母を用いた有用物質生産 | |
| BR112017001542B1 (pt) | Levedura recombinante produtora de acetoína, uso desta e método para produzir acetoína | |
| BR112017001539B1 (pt) | Levedura recombinante produtora de 2,3-butanodiol, uso desta e método para produzir 2,3-butanodiol | |
| WO2024040001A1 (en) | Genetically modified yeast and fermentation processes for the production of ethanol | |
| CN113795503A (zh) | 细胞色素b2在酵母中过表达用于增加乙醇生产 | |
| WO2018136385A1 (en) | Modified yeast cells that overexpress a dna polymerase subunit |
Legal Events
| Date | Code | Title | Description |
|---|---|---|---|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20170327 |
|
| A621 | Written request for application examination |
Free format text: JAPANESE INTERMEDIATE CODE: A621 Effective date: 20180521 |
|
| A131 | Notification of reasons for refusal |
Free format text: JAPANESE INTERMEDIATE CODE: A131 Effective date: 20190507 |
|
| A601 | Written request for extension of time |
Free format text: JAPANESE INTERMEDIATE CODE: A601 Effective date: 20190726 |
|
| A601 | Written request for extension of time |
Free format text: JAPANESE INTERMEDIATE CODE: A601 Effective date: 20191004 |
|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20191107 |
|
| A02 | Decision of refusal |
Free format text: JAPANESE INTERMEDIATE CODE: A02 Effective date: 20200413 |
|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20200813 |
|
| C60 | Trial request (containing other claim documents, opposition documents) |
Free format text: JAPANESE INTERMEDIATE CODE: C60 Effective date: 20200813 |
|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20200818 |
|
| A911 | Transfer to examiner for re-examination before appeal (zenchi) |
Free format text: JAPANESE INTERMEDIATE CODE: A911 Effective date: 20200904 |
|
| C21 | Notice of transfer of a case for reconsideration by examiners before appeal proceedings |
Free format text: JAPANESE INTERMEDIATE CODE: C21 Effective date: 20200907 |
|
| A131 | Notification of reasons for refusal |
Free format text: JAPANESE INTERMEDIATE CODE: A131 Effective date: 20201026 |
|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20201125 |
|
| TRDD | Decision of grant or rejection written | ||
| A01 | Written decision to grant a patent or to grant a registration (utility model) |
Free format text: JAPANESE INTERMEDIATE CODE: A01 Effective date: 20210208 |
|
| A61 | First payment of annual fees (during grant procedure) |
Free format text: JAPANESE INTERMEDIATE CODE: A61 Effective date: 20210302 |
|
| R150 | Certificate of patent or registration of utility model |
Ref document number: 6847036 Country of ref document: JP Free format text: JAPANESE INTERMEDIATE CODE: R150 |
|
| R250 | Receipt of annual fees |
Free format text: JAPANESE INTERMEDIATE CODE: R250 |