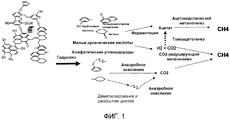
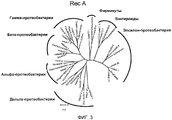
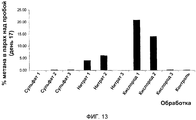
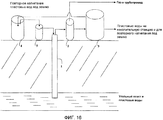
RU2488636C2 - Способы стимуляции биогенного продуцирования метана в углеводородсодержащих пластах - Google Patents
Способы стимуляции биогенного продуцирования метана в углеводородсодержащих пластах Download PDFInfo
- Publication number
- RU2488636C2 RU2488636C2 RU2010150769/10A RU2010150769A RU2488636C2 RU 2488636 C2 RU2488636 C2 RU 2488636C2 RU 2010150769/10 A RU2010150769/10 A RU 2010150769/10A RU 2010150769 A RU2010150769 A RU 2010150769A RU 2488636 C2 RU2488636 C2 RU 2488636C2
- Authority
- RU
- Russia
- Prior art keywords
- methane
- coal
- microorganisms
- hydrocarbon
- production
- Prior art date
Links
- VNWKTOKETHGBQD-UHFFFAOYSA-N methane Chemical compound C VNWKTOKETHGBQD-UHFFFAOYSA-N 0.000 title claims abstract description 391
- 238000000034 method Methods 0.000 title claims abstract description 111
- 229930195733 hydrocarbon Natural products 0.000 title claims abstract description 103
- 150000002430 hydrocarbons Chemical class 0.000 title claims abstract description 103
- 239000004215 Carbon black (E152) Substances 0.000 title claims abstract description 83
- 230000000035 biogenic effect Effects 0.000 title claims abstract description 34
- 244000005700 microbiome Species 0.000 claims abstract description 161
- 238000004519 manufacturing process Methods 0.000 claims abstract description 86
- 102000004157 Hydrolases Human genes 0.000 claims abstract description 74
- 108090000604 Hydrolases Proteins 0.000 claims abstract description 74
- 125000003147 glycosyl group Chemical group 0.000 claims abstract description 65
- 108090000623 proteins and genes Proteins 0.000 claims abstract description 57
- -1 etherases Proteins 0.000 claims abstract description 24
- 239000000758 substrate Substances 0.000 claims abstract description 24
- 102000004020 Oxygenases Human genes 0.000 claims abstract description 22
- 108090000417 Oxygenases Proteins 0.000 claims abstract description 22
- 239000000376 reactant Substances 0.000 claims abstract description 18
- 230000004060 metabolic process Effects 0.000 claims abstract description 17
- 108010074633 Mixed Function Oxygenases Proteins 0.000 claims abstract description 13
- 102000008109 Mixed Function Oxygenases Human genes 0.000 claims abstract description 13
- 102000004316 Oxidoreductases Human genes 0.000 claims abstract description 12
- 108090000854 Oxidoreductases Proteins 0.000 claims abstract description 12
- 108010028143 Dioxygenases Proteins 0.000 claims abstract description 11
- 102000016680 Dioxygenases Human genes 0.000 claims abstract description 11
- 150000007523 nucleic acids Chemical class 0.000 claims abstract description 11
- 108090000371 Esterases Proteins 0.000 claims abstract description 8
- 108010020056 Hydrogenase Proteins 0.000 claims abstract description 6
- 108010029541 Laccase Proteins 0.000 claims abstract description 6
- 108700020962 Peroxidase Proteins 0.000 claims abstract description 6
- 102000003992 Peroxidases Human genes 0.000 claims abstract description 6
- 108060008724 Tyrosinase Proteins 0.000 claims abstract description 6
- 102000003425 Tyrosinase Human genes 0.000 claims abstract description 6
- 108090000637 alpha-Amylases Proteins 0.000 claims abstract description 6
- 108010025188 Alcohol oxidase Proteins 0.000 claims abstract description 5
- 108010053835 Catalase Proteins 0.000 claims abstract description 5
- 102000016938 Catalase Human genes 0.000 claims abstract description 5
- 108010084185 Cellulases Proteins 0.000 claims abstract description 5
- 102000005575 Cellulases Human genes 0.000 claims abstract description 5
- 108010020943 Nitrogenase Proteins 0.000 claims abstract description 5
- 108010056856 methyl coenzyme M methylreductase Proteins 0.000 claims abstract description 5
- 108010065511 Amylases Proteins 0.000 claims abstract description 4
- 102000013142 Amylases Human genes 0.000 claims abstract description 4
- 108091007187 Reductases Proteins 0.000 claims abstract description 4
- 235000019418 amylase Nutrition 0.000 claims abstract description 4
- 229940025131 amylases Drugs 0.000 claims abstract description 4
- 239000003245 coal Substances 0.000 claims description 113
- 230000015572 biosynthetic process Effects 0.000 claims description 94
- 102000004190 Enzymes Human genes 0.000 claims description 72
- 108090000790 Enzymes Proteins 0.000 claims description 72
- 229940088598 enzyme Drugs 0.000 claims description 72
- 230000000813 microbial effect Effects 0.000 claims description 50
- 241000894006 Bacteria Species 0.000 claims description 46
- 229910052760 oxygen Inorganic materials 0.000 claims description 39
- QVGXLLKOCUKJST-UHFFFAOYSA-N atomic oxygen Chemical compound [O] QVGXLLKOCUKJST-UHFFFAOYSA-N 0.000 claims description 38
- 239000001301 oxygen Substances 0.000 claims description 38
- 238000006243 chemical reaction Methods 0.000 claims description 28
- 229910052799 carbon Inorganic materials 0.000 claims description 20
- 239000007789 gas Substances 0.000 claims description 20
- OKTJSMMVPCPJKN-UHFFFAOYSA-N Carbon Chemical compound [C] OKTJSMMVPCPJKN-UHFFFAOYSA-N 0.000 claims description 19
- 239000003921 oil Substances 0.000 claims description 19
- 241000589516 Pseudomonas Species 0.000 claims description 16
- 241000894007 species Species 0.000 claims description 15
- QTBSBXVTEAMEQO-UHFFFAOYSA-M Acetate Chemical compound CC([O-])=O QTBSBXVTEAMEQO-UHFFFAOYSA-M 0.000 claims description 10
- 241000203069 Archaea Species 0.000 claims description 10
- 241000605716 Desulfovibrio Species 0.000 claims description 10
- 241000605809 Desulfuromonas Species 0.000 claims description 10
- 241001464942 Thauera Species 0.000 claims description 10
- 150000001875 compounds Chemical class 0.000 claims description 10
- 241000205017 Methanolobus Species 0.000 claims description 9
- 108091028043 Nucleic acid sequence Proteins 0.000 claims description 9
- 241000203024 Acholeplasma Species 0.000 claims description 8
- 241000193403 Clostridium Species 0.000 claims description 8
- 241001233112 Methanocalculus Species 0.000 claims description 8
- 241000863392 Pelobacter Species 0.000 claims description 8
- 241000589973 Spirochaeta Species 0.000 claims description 8
- 241001135163 Arcobacter Species 0.000 claims description 7
- 241000186811 Erysipelothrix Species 0.000 claims description 7
- LFQSCWFLJHTTHZ-UHFFFAOYSA-N Ethanol Chemical compound CCO LFQSCWFLJHTTHZ-UHFFFAOYSA-N 0.000 claims description 6
- 239000003415 peat Substances 0.000 claims description 6
- 230000002195 synergetic effect Effects 0.000 claims description 6
- 239000003077 lignite Substances 0.000 claims description 5
- 229910052698 phosphorus Inorganic materials 0.000 claims description 5
- 239000011574 phosphorus Substances 0.000 claims description 5
- 230000009467 reduction Effects 0.000 claims description 5
- 238000012360 testing method Methods 0.000 claims description 5
- 239000011573 trace mineral Substances 0.000 claims description 5
- 235000013619 trace mineral Nutrition 0.000 claims description 5
- 241000721720 Magnetospirillum Species 0.000 claims description 4
- OAICVXFJPJFONN-UHFFFAOYSA-N Phosphorus Chemical compound [P] OAICVXFJPJFONN-UHFFFAOYSA-N 0.000 claims description 4
- 241000580834 Sulfurospirillum Species 0.000 claims description 4
- 150000001335 aliphatic alkanes Chemical class 0.000 claims description 4
- 150000001412 amines Chemical class 0.000 claims description 4
- 150000004945 aromatic hydrocarbons Chemical class 0.000 claims description 4
- 238000000338 in vitro Methods 0.000 claims description 4
- 229910052751 metal Inorganic materials 0.000 claims description 4
- 239000002184 metal Substances 0.000 claims description 4
- 150000007524 organic acids Chemical class 0.000 claims description 4
- 150000003573 thiols Chemical class 0.000 claims description 4
- HIXDQWDOVZUNNA-UHFFFAOYSA-N 2-(3,4-dimethoxyphenyl)-5-hydroxy-7-methoxychromen-4-one Chemical compound C=1C(OC)=CC(O)=C(C(C=2)=O)C=1OC=2C1=CC=C(OC)C(OC)=C1 HIXDQWDOVZUNNA-UHFFFAOYSA-N 0.000 claims description 3
- NINIDFKCEFEMDL-UHFFFAOYSA-N Sulfur Chemical compound [S] NINIDFKCEFEMDL-UHFFFAOYSA-N 0.000 claims description 3
- 150000001299 aldehydes Chemical class 0.000 claims description 3
- 150000001336 alkenes Chemical class 0.000 claims description 3
- 150000001491 aromatic compounds Chemical class 0.000 claims description 3
- RTZKZFJDLAIYFH-UHFFFAOYSA-N ether Substances CCOCC RTZKZFJDLAIYFH-UHFFFAOYSA-N 0.000 claims description 3
- 239000000295 fuel oil Substances 0.000 claims description 3
- 229910052736 halogen Inorganic materials 0.000 claims description 3
- 150000002367 halogens Chemical class 0.000 claims description 3
- 150000002576 ketones Chemical class 0.000 claims description 3
- 239000011593 sulfur Substances 0.000 claims description 3
- 229910052717 sulfur Inorganic materials 0.000 claims description 3
- 239000011269 tar Substances 0.000 claims description 3
- 230000037361 pathway Effects 0.000 claims description 2
- 238000012216 screening Methods 0.000 claims description 2
- 241000605008 Spirillum Species 0.000 claims 1
- 150000001345 alkine derivatives Chemical class 0.000 claims 1
- 229910052739 hydrogen Inorganic materials 0.000 abstract description 12
- 239000001257 hydrogen Substances 0.000 abstract description 11
- 239000000126 substance Substances 0.000 abstract description 10
- UFHFLCQGNIYNRP-UHFFFAOYSA-N Hydrogen Chemical compound [H][H] UFHFLCQGNIYNRP-UHFFFAOYSA-N 0.000 abstract description 8
- 230000000694 effects Effects 0.000 abstract description 7
- 108020004707 nucleic acids Proteins 0.000 abstract description 5
- 102000039446 nucleic acids Human genes 0.000 abstract description 5
- 230000009466 transformation Effects 0.000 abstract description 3
- 238000005755 formation reaction Methods 0.000 description 78
- 239000000021 stimulant Substances 0.000 description 26
- ROSDSFDQCJNGOL-UHFFFAOYSA-N Dimethylamine Chemical compound CNC ROSDSFDQCJNGOL-UHFFFAOYSA-N 0.000 description 23
- 239000008398 formation water Substances 0.000 description 23
- XLYOFNOQVPJJNP-UHFFFAOYSA-N water Substances O XLYOFNOQVPJJNP-UHFFFAOYSA-N 0.000 description 22
- 108020004414 DNA Proteins 0.000 description 20
- 230000037353 metabolic pathway Effects 0.000 description 19
- 102000004169 proteins and genes Human genes 0.000 description 19
- OKKJLVBELUTLKV-UHFFFAOYSA-N Methanol Chemical compound OC OKKJLVBELUTLKV-UHFFFAOYSA-N 0.000 description 18
- 235000018102 proteins Nutrition 0.000 description 17
- 238000003776 cleavage reaction Methods 0.000 description 16
- 230000006870 function Effects 0.000 description 16
- 238000011065 in-situ storage Methods 0.000 description 16
- 239000000047 product Substances 0.000 description 16
- 230000007017 scission Effects 0.000 description 16
- 230000004936 stimulating effect Effects 0.000 description 16
- 230000000638 stimulation Effects 0.000 description 16
- 210000004899 c-terminal region Anatomy 0.000 description 14
- 238000000354 decomposition reaction Methods 0.000 description 13
- 239000000203 mixture Substances 0.000 description 13
- 230000001580 bacterial effect Effects 0.000 description 12
- 210000004027 cell Anatomy 0.000 description 12
- 230000007613 environmental effect Effects 0.000 description 12
- 239000002609 medium Substances 0.000 description 12
- 108010038196 saccharide-binding proteins Proteins 0.000 description 12
- 238000004458 analytical method Methods 0.000 description 10
- 239000012634 fragment Substances 0.000 description 10
- UHOVQNZJYSORNB-UHFFFAOYSA-N Benzene Chemical compound C1=CC=CC=C1 UHOVQNZJYSORNB-UHFFFAOYSA-N 0.000 description 9
- 230000000696 methanogenic effect Effects 0.000 description 9
- 230000008569 process Effects 0.000 description 9
- 238000012163 sequencing technique Methods 0.000 description 9
- 108010004964 Tetrahydromethanopterin S-methyltransferase Proteins 0.000 description 8
- 238000013459 approach Methods 0.000 description 8
- 239000003795 chemical substances by application Substances 0.000 description 8
- 238000003860 storage Methods 0.000 description 8
- IJGRMHOSHXDMSA-UHFFFAOYSA-N Atomic nitrogen Chemical compound N#N IJGRMHOSHXDMSA-UHFFFAOYSA-N 0.000 description 7
- 230000002255 enzymatic effect Effects 0.000 description 7
- 230000012010 growth Effects 0.000 description 7
- 238000002347 injection Methods 0.000 description 7
- 239000007924 injection Substances 0.000 description 7
- QMMFVYPAHWMCMS-UHFFFAOYSA-N Dimethyl sulfide Chemical compound CSC QMMFVYPAHWMCMS-UHFFFAOYSA-N 0.000 description 6
- BAVYZALUXZFZLV-UHFFFAOYSA-N Methylamine Chemical compound NC BAVYZALUXZFZLV-UHFFFAOYSA-N 0.000 description 6
- FAPWRFPIFSIZLT-UHFFFAOYSA-M Sodium chloride Chemical compound [Na+].[Cl-] FAPWRFPIFSIZLT-UHFFFAOYSA-M 0.000 description 6
- YXFVVABEGXRONW-UHFFFAOYSA-N Toluene Chemical compound CC1=CC=CC=C1 YXFVVABEGXRONW-UHFFFAOYSA-N 0.000 description 6
- 239000000370 acceptor Substances 0.000 description 6
- 125000003118 aryl group Chemical group 0.000 description 6
- 230000003197 catalytic effect Effects 0.000 description 6
- 238000012512 characterization method Methods 0.000 description 6
- 238000011066 ex-situ storage Methods 0.000 description 6
- 238000000605 extraction Methods 0.000 description 6
- 239000012530 fluid Substances 0.000 description 6
- 108010050441 methyl coenzyme M reductase Proteins 0.000 description 6
- 239000002245 particle Substances 0.000 description 6
- 239000011435 rock Substances 0.000 description 6
- 238000005070 sampling Methods 0.000 description 6
- GETQZCLCWQTVFV-UHFFFAOYSA-N trimethylamine Chemical compound CN(C)C GETQZCLCWQTVFV-UHFFFAOYSA-N 0.000 description 6
- 239000003643 water by type Substances 0.000 description 6
- PEDCQBHIVMGVHV-UHFFFAOYSA-N Glycerine Chemical compound OCC(O)CO PEDCQBHIVMGVHV-UHFFFAOYSA-N 0.000 description 5
- XEEYBQQBJWHFJM-UHFFFAOYSA-N Iron Chemical compound [Fe] XEEYBQQBJWHFJM-UHFFFAOYSA-N 0.000 description 5
- KFZMGEQAYNKOFK-UHFFFAOYSA-N Isopropanol Chemical compound CC(C)O KFZMGEQAYNKOFK-UHFFFAOYSA-N 0.000 description 5
- QAOWNCQODCNURD-UHFFFAOYSA-L Sulfate Chemical compound [O-]S([O-])(=O)=O QAOWNCQODCNURD-UHFFFAOYSA-L 0.000 description 5
- 239000001913 cellulose Substances 0.000 description 5
- 229920002678 cellulose Polymers 0.000 description 5
- 238000005520 cutting process Methods 0.000 description 5
- 238000000855 fermentation Methods 0.000 description 5
- 230000004151 fermentation Effects 0.000 description 5
- 229910052500 inorganic mineral Inorganic materials 0.000 description 5
- 230000002503 metabolic effect Effects 0.000 description 5
- 239000011707 mineral Substances 0.000 description 5
- 235000010755 mineral Nutrition 0.000 description 5
- 239000005416 organic matter Substances 0.000 description 5
- 125000005575 polycyclic aromatic hydrocarbon group Chemical group 0.000 description 5
- 239000004576 sand Substances 0.000 description 5
- 108020004465 16S ribosomal RNA Proteins 0.000 description 4
- QGZKDVFQNNGYKY-UHFFFAOYSA-N Ammonia Chemical compound N QGZKDVFQNNGYKY-UHFFFAOYSA-N 0.000 description 4
- 102100026189 Beta-galactosidase Human genes 0.000 description 4
- CURLTUGMZLYLDI-UHFFFAOYSA-N Carbon dioxide Chemical compound O=C=O CURLTUGMZLYLDI-UHFFFAOYSA-N 0.000 description 4
- XTEGARKTQYYJKE-UHFFFAOYSA-M Chlorate Chemical compound [O-]Cl(=O)=O XTEGARKTQYYJKE-UHFFFAOYSA-M 0.000 description 4
- BDAGIHXWWSANSR-UHFFFAOYSA-M Formate Chemical compound [O-]C=O BDAGIHXWWSANSR-UHFFFAOYSA-M 0.000 description 4
- 241000233866 Fungi Species 0.000 description 4
- LSDPWZHWYPCBBB-UHFFFAOYSA-N Methanethiol Chemical compound SC LSDPWZHWYPCBBB-UHFFFAOYSA-N 0.000 description 4
- 229910002651 NO3 Inorganic materials 0.000 description 4
- NHNBFGGVMKEFGY-UHFFFAOYSA-N Nitrate Chemical compound [O-][N+]([O-])=O NHNBFGGVMKEFGY-UHFFFAOYSA-N 0.000 description 4
- 241000204652 Thermotoga Species 0.000 description 4
- ZSLZBFCDCINBPY-ZSJPKINUSA-N acetyl-CoA Chemical compound O[C@@H]1[C@H](OP(O)(O)=O)[C@@H](COP(O)(=O)OP(O)(=O)OCC(C)(C)[C@@H](O)C(=O)NCCC(=O)NCCSC(=O)C)O[C@H]1N1C2=NC=NC(N)=C2N=C1 ZSLZBFCDCINBPY-ZSJPKINUSA-N 0.000 description 4
- 102000004139 alpha-Amylases Human genes 0.000 description 4
- 229940024171 alpha-amylase Drugs 0.000 description 4
- 108010005774 beta-Galactosidase Proteins 0.000 description 4
- 229940041514 candida albicans extract Drugs 0.000 description 4
- 239000003575 carbonaceous material Substances 0.000 description 4
- 238000004113 cell culture Methods 0.000 description 4
- 239000000499 gel Substances 0.000 description 4
- 230000002068 genetic effect Effects 0.000 description 4
- 238000011331 genomic analysis Methods 0.000 description 4
- 238000002955 isolation Methods 0.000 description 4
- 239000003345 natural gas Substances 0.000 description 4
- 235000015097 nutrients Nutrition 0.000 description 4
- 230000003647 oxidation Effects 0.000 description 4
- 238000007254 oxidation reaction Methods 0.000 description 4
- 230000035699 permeability Effects 0.000 description 4
- 239000002689 soil Substances 0.000 description 4
- 239000007787 solid Substances 0.000 description 4
- 239000000243 solution Substances 0.000 description 4
- 239000012138 yeast extract Substances 0.000 description 4
- 229920001817 Agar Polymers 0.000 description 3
- 108010061397 Ammonia monooxygenase Proteins 0.000 description 3
- 241000726110 Azoarcus Species 0.000 description 3
- 241001112695 Clostridiales Species 0.000 description 3
- 241000588724 Escherichia coli Species 0.000 description 3
- XUJNEKJLAYXESH-REOHCLBHSA-N L-Cysteine Chemical compound SC[C@H](N)C(O)=O XUJNEKJLAYXESH-REOHCLBHSA-N 0.000 description 3
- 241000205276 Methanosarcina Species 0.000 description 3
- 241000205011 Methanothrix Species 0.000 description 3
- 240000004808 Saccharomyces cerevisiae Species 0.000 description 3
- 241001234687 Thermacetogenium Species 0.000 description 3
- 238000009825 accumulation Methods 0.000 description 3
- 108010093941 acetylxylan esterase Proteins 0.000 description 3
- 239000008272 agar Substances 0.000 description 3
- 108010084650 alpha-N-arabinofuranosidase Proteins 0.000 description 3
- 239000012298 atmosphere Substances 0.000 description 3
- 239000011324 bead Substances 0.000 description 3
- WPYMKLBDIGXBTP-UHFFFAOYSA-N benzoic acid Chemical compound OC(=O)C1=CC=CC=C1 WPYMKLBDIGXBTP-UHFFFAOYSA-N 0.000 description 3
- 108010080434 cephalosporin-C deacetylase Proteins 0.000 description 3
- 229960002433 cysteine Drugs 0.000 description 3
- 230000009088 enzymatic function Effects 0.000 description 3
- 230000009483 enzymatic pathway Effects 0.000 description 3
- 150000002431 hydrogen Chemical class 0.000 description 3
- 230000007062 hydrolysis Effects 0.000 description 3
- 238000006460 hydrolysis reaction Methods 0.000 description 3
- 230000033444 hydroxylation Effects 0.000 description 3
- 238000005805 hydroxylation reaction Methods 0.000 description 3
- 238000011081 inoculation Methods 0.000 description 3
- 239000000543 intermediate Substances 0.000 description 3
- 229910000398 iron phosphate Inorganic materials 0.000 description 3
- WBJZTOZJJYAKHQ-UHFFFAOYSA-K iron(3+) phosphate Chemical compound [Fe+3].[O-]P([O-])([O-])=O WBJZTOZJJYAKHQ-UHFFFAOYSA-K 0.000 description 3
- 239000007788 liquid Substances 0.000 description 3
- 239000012139 lysis buffer Substances 0.000 description 3
- 239000000463 material Substances 0.000 description 3
- 230000007246 mechanism Effects 0.000 description 3
- 239000012528 membrane Substances 0.000 description 3
- 239000002207 metabolite Substances 0.000 description 3
- 229910052757 nitrogen Inorganic materials 0.000 description 3
- 239000008188 pellet Substances 0.000 description 3
- 108010027388 phenol 2-monooxygenase Proteins 0.000 description 3
- 239000013612 plasmid Substances 0.000 description 3
- 238000005086 pumping Methods 0.000 description 3
- 230000027756 respiratory electron transport chain Effects 0.000 description 3
- 230000029058 respiratory gaseous exchange Effects 0.000 description 3
- 238000007142 ring opening reaction Methods 0.000 description 3
- 238000000926 separation method Methods 0.000 description 3
- 239000011780 sodium chloride Substances 0.000 description 3
- 230000035882 stress Effects 0.000 description 3
- 239000006228 supernatant Substances 0.000 description 3
- 241001148471 unidentified anaerobic bacterium Species 0.000 description 3
- YBJHBAHKTGYVGT-ZKWXMUAHSA-N (+)-Biotin Chemical compound N1C(=O)N[C@@H]2[C@H](CCCCC(=O)O)SC[C@@H]21 YBJHBAHKTGYVGT-ZKWXMUAHSA-N 0.000 description 2
- VOXZDWNPVJITMN-ZBRFXRBCSA-N 17β-estradiol Chemical group OC1=CC=C2[C@H]3CC[C@](C)([C@H](CC4)O)[C@@H]4[C@@H]3CCC2=C1 VOXZDWNPVJITMN-ZBRFXRBCSA-N 0.000 description 2
- HZAXFHJVJLSVMW-UHFFFAOYSA-N 2-Aminoethan-1-ol Chemical compound NCCO HZAXFHJVJLSVMW-UHFFFAOYSA-N 0.000 description 2
- WJXSWCUQABXPFS-UHFFFAOYSA-N 3-hydroxyanthranilic acid Chemical compound NC1=C(O)C=CC=C1C(O)=O WJXSWCUQABXPFS-UHFFFAOYSA-N 0.000 description 2
- ALYNCZNDIQEVRV-UHFFFAOYSA-N 4-aminobenzoic acid Chemical compound NC1=CC=C(C(O)=O)C=C1 ALYNCZNDIQEVRV-UHFFFAOYSA-N 0.000 description 2
- 108010089063 4-hydroxybenzoate decarboxylase Proteins 0.000 description 2
- 241000590020 Achromobacter Species 0.000 description 2
- 241000607534 Aeromonas Species 0.000 description 2
- 102100040894 Amylo-alpha-1,6-glucosidase Human genes 0.000 description 2
- CIWBSHSKHKDKBQ-JLAZNSOCSA-N Ascorbic acid Chemical compound OC[C@H](O)[C@H]1OC(=O)C(O)=C1O CIWBSHSKHKDKBQ-JLAZNSOCSA-N 0.000 description 2
- 241001312727 Azospira Species 0.000 description 2
- 241000692822 Bacteroidales Species 0.000 description 2
- 241000589171 Bradyrhizobium sp. Species 0.000 description 2
- OYPRJOBELJOOCE-UHFFFAOYSA-N Calcium Chemical compound [Ca] OYPRJOBELJOOCE-UHFFFAOYSA-N 0.000 description 2
- 241000121248 Candidatus Magnetobacterium Species 0.000 description 2
- 108090000489 Carboxy-Lyases Proteins 0.000 description 2
- 108010066997 Catechol 1,2-dioxygenase Proteins 0.000 description 2
- 229920002101 Chitin Polymers 0.000 description 2
- HEDRZPFGACZZDS-UHFFFAOYSA-N Chloroform Chemical compound ClC(Cl)Cl HEDRZPFGACZZDS-UHFFFAOYSA-N 0.000 description 2
- 101710156809 DNA ligase B Proteins 0.000 description 2
- 241000188738 Desulfurococcales Species 0.000 description 2
- 241000863390 Dictyoglomus Species 0.000 description 2
- MYMOFIZGZYHOMD-UHFFFAOYSA-N Dioxygen Chemical group O=O MYMOFIZGZYHOMD-UHFFFAOYSA-N 0.000 description 2
- KCXVZYZYPLLWCC-UHFFFAOYSA-N EDTA Chemical compound OC(=O)CN(CC(O)=O)CCN(CC(O)=O)CC(O)=O KCXVZYZYPLLWCC-UHFFFAOYSA-N 0.000 description 2
- DHMQDGOQFOQNFH-UHFFFAOYSA-N Glycine Chemical compound NCC(O)=O DHMQDGOQFOQNFH-UHFFFAOYSA-N 0.000 description 2
- 102000004195 Isomerases Human genes 0.000 description 2
- 108090000769 Isomerases Proteins 0.000 description 2
- 108010090665 Mannosyl-Glycoprotein Endo-beta-N-Acetylglucosaminidase Proteins 0.000 description 2
- 241000203067 Methanobacteriales Species 0.000 description 2
- 241000202974 Methanobacterium Species 0.000 description 2
- 241000203361 Methanococcales Species 0.000 description 2
- 241000959683 Methanopyrales Species 0.000 description 2
- 241000205274 Methanosarcina mazei Species 0.000 description 2
- 241001302035 Methanothermobacter Species 0.000 description 2
- PVNIIMVLHYAWGP-UHFFFAOYSA-N Niacin Chemical compound OC(=O)C1=CC=CN=C1 PVNIIMVLHYAWGP-UHFFFAOYSA-N 0.000 description 2
- 241001078793 Niastella Species 0.000 description 2
- 108700026244 Open Reading Frames Proteins 0.000 description 2
- 229910019142 PO4 Inorganic materials 0.000 description 2
- 241000315730 Pannonibacter Species 0.000 description 2
- 241001135648 Petrotoga Species 0.000 description 2
- ISWSIDIOOBJBQZ-UHFFFAOYSA-N Phenol Chemical compound OC1=CC=CC=C1 ISWSIDIOOBJBQZ-UHFFFAOYSA-N 0.000 description 2
- 241000589963 Planctomycetaceae Species 0.000 description 2
- ZLMJMSJWJFRBEC-UHFFFAOYSA-N Potassium Chemical compound [K] ZLMJMSJWJFRBEC-UHFFFAOYSA-N 0.000 description 2
- 241001161494 Proteiniphilum Species 0.000 description 2
- 241000192142 Proteobacteria Species 0.000 description 2
- 241000514830 Pseudomonas entomophila L48 Species 0.000 description 2
- LCTONWCANYUPML-UHFFFAOYSA-M Pyruvate Chemical compound CC(=O)C([O-])=O LCTONWCANYUPML-UHFFFAOYSA-M 0.000 description 2
- 108010055016 Rec A Recombinases Proteins 0.000 description 2
- AUNGANRZJHBGPY-SCRDCRAPSA-N Riboflavin Chemical compound OC[C@@H](O)[C@@H](O)[C@@H](O)CN1C=2C=C(C)C(C)=CC=2N=C2C1=NC(=O)NC2=O AUNGANRZJHBGPY-SCRDCRAPSA-N 0.000 description 2
- 241000095588 Ruminococcaceae Species 0.000 description 2
- 241000425108 Thalassospira Species 0.000 description 2
- 241001135707 Thermodesulfovibrio Species 0.000 description 2
- 241001074901 Thermoprotei Species 0.000 description 2
- 108010075474 Toluene dioxygenase Proteins 0.000 description 2
- 239000007983 Tris buffer Substances 0.000 description 2
- 230000009471 action Effects 0.000 description 2
- 239000000654 additive Substances 0.000 description 2
- 150000001337 aliphatic alkines Chemical class 0.000 description 2
- 229910021529 ammonia Inorganic materials 0.000 description 2
- 230000004099 anaerobic respiration Effects 0.000 description 2
- 210000004436 artificial bacterial chromosome Anatomy 0.000 description 2
- 239000005420 bog Substances 0.000 description 2
- 239000006227 byproduct Substances 0.000 description 2
- 239000011575 calcium Substances 0.000 description 2
- 229910052791 calcium Inorganic materials 0.000 description 2
- 235000001465 calcium Nutrition 0.000 description 2
- 229910002092 carbon dioxide Inorganic materials 0.000 description 2
- 239000001569 carbon dioxide Substances 0.000 description 2
- 108010031234 carbon monoxide dehydrogenase Proteins 0.000 description 2
- 230000015556 catabolic process Effects 0.000 description 2
- YCIMNLLNPGFGHC-UHFFFAOYSA-N catechol Chemical compound OC1=CC=CC=C1O YCIMNLLNPGFGHC-UHFFFAOYSA-N 0.000 description 2
- 230000035606 childbirth Effects 0.000 description 2
- 238000010367 cloning Methods 0.000 description 2
- 238000000576 coating method Methods 0.000 description 2
- 108010066199 coenzyme F420 hydrogenase Proteins 0.000 description 2
- XUJNEKJLAYXESH-UHFFFAOYSA-N cysteine Natural products SCC(N)C(O)=O XUJNEKJLAYXESH-UHFFFAOYSA-N 0.000 description 2
- 235000018417 cysteine Nutrition 0.000 description 2
- OPTASPLRGRRNAP-UHFFFAOYSA-N cytosine Chemical compound NC=1C=CNC(=O)N=1 OPTASPLRGRRNAP-UHFFFAOYSA-N 0.000 description 2
- 238000004821 distillation Methods 0.000 description 2
- 150000004141 diterpene derivatives Chemical class 0.000 description 2
- 238000005553 drilling Methods 0.000 description 2
- 230000002708 enhancing effect Effects 0.000 description 2
- 229960005309 estradiol Drugs 0.000 description 2
- 229930182833 estradiol Natural products 0.000 description 2
- 210000003527 eukaryotic cell Anatomy 0.000 description 2
- OVBPIULPVIDEAO-LBPRGKRZSA-N folic acid Chemical compound C=1N=C2NC(N)=NC(=O)C2=NC=1CNC1=CC=C(C(=O)N[C@@H](CCC(O)=O)C(O)=O)C=C1 OVBPIULPVIDEAO-LBPRGKRZSA-N 0.000 description 2
- 108010001852 formylmethanofuran-tetrahydromethanopterin formyltransferase Proteins 0.000 description 2
- 238000004817 gas chromatography Methods 0.000 description 2
- 238000012268 genome sequencing Methods 0.000 description 2
- 239000011521 glass Substances 0.000 description 2
- 235000011187 glycerol Nutrition 0.000 description 2
- UYTPUPDQBNUYGX-UHFFFAOYSA-N guanine Chemical compound O=C1NC(N)=NC2=C1N=CN2 UYTPUPDQBNUYGX-UHFFFAOYSA-N 0.000 description 2
- 230000003301 hydrolyzing effect Effects 0.000 description 2
- 230000006872 improvement Effects 0.000 description 2
- 238000010952 in-situ formation Methods 0.000 description 2
- 238000011534 incubation Methods 0.000 description 2
- 229910052742 iron Inorganic materials 0.000 description 2
- JVTAAEKCZFNVCJ-UHFFFAOYSA-N lactic acid Chemical compound CC(O)C(O)=O JVTAAEKCZFNVCJ-UHFFFAOYSA-N 0.000 description 2
- 229910052748 manganese Inorganic materials 0.000 description 2
- 239000011572 manganese Substances 0.000 description 2
- 125000002496 methyl group Chemical group [H]C([H])([H])* 0.000 description 2
- 108010072855 methylenetetrahydromethanopterin dehydrogenase Proteins 0.000 description 2
- 239000012452 mother liquor Substances 0.000 description 2
- 108020003068 nitronate monooxygenase Proteins 0.000 description 2
- NBIIXXVUZAFLBC-UHFFFAOYSA-K phosphate Chemical compound [O-]P([O-])([O-])=O NBIIXXVUZAFLBC-UHFFFAOYSA-K 0.000 description 2
- 239000010452 phosphate Substances 0.000 description 2
- 238000003752 polymerase chain reaction Methods 0.000 description 2
- 239000011591 potassium Substances 0.000 description 2
- 229910052700 potassium Inorganic materials 0.000 description 2
- 239000013587 production medium Substances 0.000 description 2
- 238000011084 recovery Methods 0.000 description 2
- 230000004044 response Effects 0.000 description 2
- NRJQGHHZMSOUEN-HZLKACBZSA-N s-[2-[3-[[(2r)-4-[[[(2r,3s,4r,5r)-5-(6-aminopurin-9-yl)-4-hydroxy-3-phosphonooxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-hydroxyphosphoryl]oxy-2-hydroxy-3,3-dimethylbutanoyl]amino]propanoylamino]ethyl] (3s,7r,11r)-3,7,11,15-tetramethylhexadecanethioate Chemical compound O[C@@H]1[C@H](OP(O)(O)=O)[C@@H](COP(O)(=O)OP(O)(=O)OCC(C)(C)[C@@H](O)C(=O)NCCC(=O)NCCSC(=O)C[C@@H](C)CCC[C@H](C)CCC[C@H](C)CCCC(C)C)O[C@H]1N1C2=NC=NC(N)=C2N=C1 NRJQGHHZMSOUEN-HZLKACBZSA-N 0.000 description 2
- 239000010802 sludge Substances 0.000 description 2
- 239000011734 sodium Substances 0.000 description 2
- VWDWKYIASSYTQR-UHFFFAOYSA-N sodium nitrate Chemical compound [Na+].[O-][N+]([O-])=O VWDWKYIASSYTQR-UHFFFAOYSA-N 0.000 description 2
- ATHGHQPFGPMSJY-UHFFFAOYSA-N spermidine Chemical compound NCCCCNCCCN ATHGHQPFGPMSJY-UHFFFAOYSA-N 0.000 description 2
- 238000010561 standard procedure Methods 0.000 description 2
- 239000000725 suspension Substances 0.000 description 2
- XOAAWQZATWQOTB-UHFFFAOYSA-N taurine Chemical compound NCCS(O)(=O)=O XOAAWQZATWQOTB-UHFFFAOYSA-N 0.000 description 2
- 238000011282 treatment Methods 0.000 description 2
- LENZDBCJOHFCAS-UHFFFAOYSA-N tris Chemical compound OCC(N)(CO)CO LENZDBCJOHFCAS-UHFFFAOYSA-N 0.000 description 2
- 235000013343 vitamin Nutrition 0.000 description 2
- 239000011782 vitamin Substances 0.000 description 2
- 229940088594 vitamin Drugs 0.000 description 2
- 229930003231 vitamin Natural products 0.000 description 2
- GHOKWGTUZJEAQD-ZETCQYMHSA-N (D)-(+)-Pantothenic acid Chemical compound OCC(C)(C)[C@@H](O)C(=O)NCCC(O)=O GHOKWGTUZJEAQD-ZETCQYMHSA-N 0.000 description 1
- WBYWAXJHAXSJNI-VOTSOKGWSA-M .beta-Phenylacrylic acid Natural products [O-]C(=O)\C=C\C1=CC=CC=C1 WBYWAXJHAXSJNI-VOTSOKGWSA-M 0.000 description 1
- GFVHBTOOPNJKLV-UHFFFAOYSA-N 1,2-dinitroglycerol Chemical compound [O-][N+](=O)OC(CO)CO[N+]([O-])=O GFVHBTOOPNJKLV-UHFFFAOYSA-N 0.000 description 1
- JSZOAYXJRCEYSX-UHFFFAOYSA-N 1-nitropropane Chemical compound CCC[N+]([O-])=O JSZOAYXJRCEYSX-UHFFFAOYSA-N 0.000 description 1
- 108010053957 2,4-dichlorophenoxyacetate-alpha-ketoglutarate dioxygenase Proteins 0.000 description 1
- DHCUIDTZCMREHG-UHFFFAOYSA-N 2-(carboxymethyl)-5-oxo-2,5-dihydro-2-furoic acid Chemical compound OC(=O)CC1(C(O)=O)OC(=O)C=C1 DHCUIDTZCMREHG-UHFFFAOYSA-N 0.000 description 1
- 108010043754 2-phosphosulfolactate phosphatase Proteins 0.000 description 1
- SJSOFNCYXJUNBT-UHFFFAOYSA-N 3,4,5-trimethoxybenzoic acid Chemical compound COC1=CC(C(O)=O)=CC(OC)=C1OC SJSOFNCYXJUNBT-UHFFFAOYSA-N 0.000 description 1
- 108010070279 3-carboxyethylcatechol 2,3-dioxygenase Proteins 0.000 description 1
- 108030002427 3-phenylpropanoate dioxygenases Proteins 0.000 description 1
- 108010043797 4-alpha-glucanotransferase Proteins 0.000 description 1
- 108010068327 4-hydroxyphenylpyruvate dioxygenase Proteins 0.000 description 1
- 102100028626 4-hydroxyphenylpyruvate dioxygenase Human genes 0.000 description 1
- 108010029607 4-nitrophenyl-alpha-glucosidase Proteins 0.000 description 1
- 108091006112 ATPases Proteins 0.000 description 1
- 241001468161 Acetobacterium Species 0.000 description 1
- 241000245942 Acetomicrobium Species 0.000 description 1
- 241000589291 Acinetobacter Species 0.000 description 1
- 102000057290 Adenosine Triphosphatases Human genes 0.000 description 1
- 241000611272 Alcanivorax Species 0.000 description 1
- 108020002663 Aldehyde Dehydrogenase Proteins 0.000 description 1
- 102000005369 Aldehyde Dehydrogenase Human genes 0.000 description 1
- 241001149240 Alkaliphilus metalliredigens QYMF Species 0.000 description 1
- 108030006497 Alkanesulfonate monooxygenases Proteins 0.000 description 1
- 108700023205 Allophanate hydrolases Proteins 0.000 description 1
- QGZKDVFQNNGYKY-UHFFFAOYSA-O Ammonium Chemical compound [NH4+] QGZKDVFQNNGYKY-UHFFFAOYSA-O 0.000 description 1
- 101710104691 Amylo-alpha-1,6-glucosidase Proteins 0.000 description 1
- 241001629581 Anaerosinus Species 0.000 description 1
- 241001558988 Anaerovorax Species 0.000 description 1
- 101001073434 Anopheles gambiae Peritrophin-1 Proteins 0.000 description 1
- 241000092810 Aquimonas Species 0.000 description 1
- 241001148573 Azoarcus sp. Species 0.000 description 1
- 241001312730 Azonexus Species 0.000 description 1
- 241001112741 Bacillaceae Species 0.000 description 1
- 241000193830 Bacillus <bacterium> Species 0.000 description 1
- 101000758783 Bacillus subtilis (strain 168) Probable 4-hydroxyphenylacetate 3-monooxygenase Proteins 0.000 description 1
- 241000605059 Bacteroidetes Species 0.000 description 1
- 108010022470 Benzoate 1,2-dioxygenase Proteins 0.000 description 1
- 239000005711 Benzoic acid Substances 0.000 description 1
- 241001135755 Betaproteobacteria Species 0.000 description 1
- 239000002028 Biomass Substances 0.000 description 1
- 241000555281 Brevibacillus Species 0.000 description 1
- 241001453380 Burkholderia Species 0.000 description 1
- 241001604116 Burkholderia mallei NCTC 10247 Species 0.000 description 1
- 241001604141 Burkholderia pseudomallei 1710b Species 0.000 description 1
- 241001604148 Burkholderia pseudomallei 668 Species 0.000 description 1
- 241000605902 Butyrivibrio Species 0.000 description 1
- 101150030566 CCS1 gene Proteins 0.000 description 1
- 241001041715 Caldicellulosiruptor saccharolyticus DSM 8903 Species 0.000 description 1
- 241000907319 Carnimonas Species 0.000 description 1
- 102000014914 Carrier Proteins Human genes 0.000 description 1
- 108010078791 Carrier Proteins Proteins 0.000 description 1
- 108010080972 Catechol 2,3-dioxygenase Proteins 0.000 description 1
- 108010059892 Cellulase Proteins 0.000 description 1
- 108010022172 Chitinases Proteins 0.000 description 1
- 102000012286 Chitinases Human genes 0.000 description 1
- 229920001661 Chitosan Polymers 0.000 description 1
- VEXZGXHMUGYJMC-UHFFFAOYSA-M Chloride anion Chemical compound [Cl-] VEXZGXHMUGYJMC-UHFFFAOYSA-M 0.000 description 1
- 241000999914 Chromobacterium violaceum ATCC 12472 Species 0.000 description 1
- 241000611330 Chryseobacterium Species 0.000 description 1
- 241000238855 Chrysiogenes Species 0.000 description 1
- WBYWAXJHAXSJNI-SREVYHEPSA-N Cinnamic acid Chemical compound OC(=O)\C=C/C1=CC=CC=C1 WBYWAXJHAXSJNI-SREVYHEPSA-N 0.000 description 1
- 241000588923 Citrobacter Species 0.000 description 1
- 241001112696 Clostridia Species 0.000 description 1
- 108020004705 Codon Proteins 0.000 description 1
- 101100332461 Coffea arabica DXMT2 gene Proteins 0.000 description 1
- 241000971513 Coprothermobacter Species 0.000 description 1
- 102000005297 Cytochrome P-450 CYP4A Human genes 0.000 description 1
- 108010081498 Cytochrome P-450 CYP4A Proteins 0.000 description 1
- 108010015742 Cytochrome P-450 Enzyme System Proteins 0.000 description 1
- 102000003849 Cytochrome P450 Human genes 0.000 description 1
- AUNGANRZJHBGPY-UHFFFAOYSA-N D-Lyxoflavin Natural products OCC(O)C(O)C(O)CN1C=2C=C(C)C(C)=CC=2N=C2C1=NC(=O)NC2=O AUNGANRZJHBGPY-UHFFFAOYSA-N 0.000 description 1
- 101710156804 DNA ligase A Proteins 0.000 description 1
- 241001245615 Dechloromonas Species 0.000 description 1
- 241000059188 Dechloromonas aromatica RCB Species 0.000 description 1
- 241001425580 Deferribacteraceae Species 0.000 description 1
- 241001135761 Deltaproteobacteria Species 0.000 description 1
- 102100037458 Dephospho-CoA kinase Human genes 0.000 description 1
- 241000383790 Desulfococcus oleovorans Hxd3 Species 0.000 description 1
- 241000205646 Devosia Species 0.000 description 1
- 241000024397 Dysgonomonas Species 0.000 description 1
- 241000588914 Enterobacter Species 0.000 description 1
- 241000206602 Eukaryota Species 0.000 description 1
- 241000131486 Ewingella Species 0.000 description 1
- 101710116650 FAD-dependent monooxygenase Proteins 0.000 description 1
- 241000192128 Gammaproteobacteria Species 0.000 description 1
- 241000626621 Geobacillus Species 0.000 description 1
- 101000866605 Geobacillus sp. (strain PA-9) 4-hydroxyphenylacetate 3-monooxygenase oxygenase component Proteins 0.000 description 1
- WQZGKKKJIJFFOK-GASJEMHNSA-N Glucose Natural products OC[C@H]1OC(O)[C@H](O)[C@@H](O)[C@@H]1O WQZGKKKJIJFFOK-GASJEMHNSA-N 0.000 description 1
- 102000010477 Glutathione S-transferase, N-terminal Human genes 0.000 description 1
- 108050001973 Glutathione S-transferase, N-terminal Proteins 0.000 description 1
- 239000004471 Glycine Substances 0.000 description 1
- 229930189936 Glyoxalase Natural products 0.000 description 1
- 229920002907 Guar gum Polymers 0.000 description 1
- 241000206596 Halomonas Species 0.000 description 1
- 241001252021 Halovibrio Species 0.000 description 1
- 108010003272 Hyaluronate lyase Proteins 0.000 description 1
- 102000001974 Hyaluronidases Human genes 0.000 description 1
- 241000862981 Hyphomonas Species 0.000 description 1
- 108010042653 IgA receptor Proteins 0.000 description 1
- DGAQECJNVWCQMB-PUAWFVPOSA-M Ilexoside XXIX Chemical compound C[C@@H]1CC[C@@]2(CC[C@@]3(C(=CC[C@H]4[C@]3(CC[C@@H]5[C@@]4(CC[C@@H](C5(C)C)OS(=O)(=O)[O-])C)C)[C@@H]2[C@]1(C)O)C)C(=O)O[C@H]6[C@@H]([C@H]([C@@H]([C@H](O6)CO)O)O)O.[Na+] DGAQECJNVWCQMB-PUAWFVPOSA-M 0.000 description 1
- 108010028688 Isoamylase Proteins 0.000 description 1
- 241000256602 Isoptera Species 0.000 description 1
- 241001112383 Jannaschia sp. Species 0.000 description 1
- WTDRDQBEARUVNC-LURJTMIESA-N L-DOPA Chemical compound OC(=O)[C@@H](N)CC1=CC=C(O)C(O)=C1 WTDRDQBEARUVNC-LURJTMIESA-N 0.000 description 1
- JVTAAEKCZFNVCJ-UHFFFAOYSA-M Lactate Chemical compound CC(O)C([O-])=O JVTAAEKCZFNVCJ-UHFFFAOYSA-M 0.000 description 1
- 241000589927 Leptospira borgpetersenii Species 0.000 description 1
- 241001549253 Levilinea Species 0.000 description 1
- 102000003960 Ligases Human genes 0.000 description 1
- 108090000364 Ligases Proteins 0.000 description 1
- 108010054320 Lignin peroxidase Proteins 0.000 description 1
- 101710158871 Luciferase-like monooxygenase Proteins 0.000 description 1
- FYYHWMGAXLPEAU-UHFFFAOYSA-N Magnesium Chemical compound [Mg] FYYHWMGAXLPEAU-UHFFFAOYSA-N 0.000 description 1
- PWHULOQIROXLJO-UHFFFAOYSA-N Manganese Chemical compound [Mn] PWHULOQIROXLJO-UHFFFAOYSA-N 0.000 description 1
- 108010059896 Manganese peroxidase Proteins 0.000 description 1
- 102100025315 Mannosyl-oligosaccharide glucosidase Human genes 0.000 description 1
- 241000206589 Marinobacter Species 0.000 description 1
- 108010052285 Membrane Proteins Proteins 0.000 description 1
- 102000018697 Membrane Proteins Human genes 0.000 description 1
- 102000003939 Membrane transport proteins Human genes 0.000 description 1
- 108090000301 Membrane transport proteins Proteins 0.000 description 1
- 108010063312 Metalloproteins Proteins 0.000 description 1
- 102000010750 Metalloproteins Human genes 0.000 description 1
- 241001644379 Methanocalculus pumilus Species 0.000 description 1
- 241000204999 Methanococcoides Species 0.000 description 1
- 241001148031 Methanococcoides burtonii Species 0.000 description 1
- 241000205026 Methanococcoides methylutens Species 0.000 description 1
- 241000203400 Methanocorpusculum Species 0.000 description 1
- 241001621918 Methanofollis Species 0.000 description 1
- 241000203006 Methanohalophilus Species 0.000 description 1
- 241000499062 Methanohalophilus euhalobius Species 0.000 description 1
- 241000203004 Methanohalophilus mahii Species 0.000 description 1
- 241001515935 Methanolobus oregonensis Species 0.000 description 1
- 241001515932 Methanolobus taylorii Species 0.000 description 1
- 241000205014 Methanolobus tindarius Species 0.000 description 1
- 241001515933 Methanolobus vulcani Species 0.000 description 1
- 241001450794 Methanomethylovorans Species 0.000 description 1
- 241001450793 Methanomethylovorans hollandica Species 0.000 description 1
- 241000203404 Methanomicrobiales Species 0.000 description 1
- 241000205284 Methanosarcina acetivorans Species 0.000 description 1
- 241000205275 Methanosarcina barkeri Species 0.000 description 1
- 241001515938 Methanosarcina siciliae Species 0.000 description 1
- 241000205290 Methanosarcina thermophila Species 0.000 description 1
- 241000204677 Methanosphaera Species 0.000 description 1
- 241000781379 Methanosphaera cuniculi Species 0.000 description 1
- 241000204676 Methanosphaera stadtmanae Species 0.000 description 1
- 241000205003 Methanothrix thermoacetophila Species 0.000 description 1
- 108010037361 Methenyltetrahydromethanopterin cyclohydrolase Proteins 0.000 description 1
- 241000082433 Methylobacillus flagellatus KT Species 0.000 description 1
- 241001655327 Micrococcales Species 0.000 description 1
- 241000258113 Monases Species 0.000 description 1
- 241000187488 Mycobacterium sp. Species 0.000 description 1
- OVBPIULPVIDEAO-UHFFFAOYSA-N N-Pteroyl-L-glutaminsaeure Natural products C=1N=C2NC(N)=NC(=O)C2=NC=1CNC1=CC=C(C(=O)NC(CCC(O)=O)C(O)=O)C=C1 OVBPIULPVIDEAO-UHFFFAOYSA-N 0.000 description 1
- 241000192121 Nitrospira <genus> Species 0.000 description 1
- 101710128228 O-methyltransferase Proteins 0.000 description 1
- RUVPEAOBARYHEY-ZUEOXWNTSA-N O[C@@H]1C(O[C@@H]([C@H]([C@@H]1O)O)C)OC(CC(=O)OCC)CCCCCCCCCCCCCCC Chemical compound O[C@@H]1C(O[C@@H]([C@H]([C@@H]1O)O)C)OC(CC(=O)OCC)CCCCCCCCCCCCCCC RUVPEAOBARYHEY-ZUEOXWNTSA-N 0.000 description 1
- 101710116435 Outer membrane protein Proteins 0.000 description 1
- 102000014386 PA14 domains Human genes 0.000 description 1
- 108050003408 PA14 domains Proteins 0.000 description 1
- 238000012408 PCR amplification Methods 0.000 description 1
- 241000179039 Paenibacillus Species 0.000 description 1
- 241000740708 Paludibacter Species 0.000 description 1
- 241000160321 Parabacteroides Species 0.000 description 1
- 241000601272 Parvibaculum lavamentivorans DS-1 Species 0.000 description 1
- 241001112694 Peptococcaceae Species 0.000 description 1
- 108090000608 Phosphoric Monoester Hydrolases Proteins 0.000 description 1
- 102000004160 Phosphoric Monoester Hydrolases Human genes 0.000 description 1
- 102100039421 Phytanoyl-CoA dioxygenase, peroxisomal Human genes 0.000 description 1
- 101710143274 Phytanoyl-CoA dioxygenase, peroxisomal Proteins 0.000 description 1
- 239000002202 Polyethylene glycol Substances 0.000 description 1
- 239000004353 Polyethylene glycol 8000 Substances 0.000 description 1
- 102100034014 Prolyl 3-hydroxylase 3 Human genes 0.000 description 1
- 241001430313 Propionibacteriaceae Species 0.000 description 1
- 101800004937 Protein C Proteins 0.000 description 1
- 102000002067 Protein Subunits Human genes 0.000 description 1
- 108010001267 Protein Subunits Proteins 0.000 description 1
- 108010016080 Protocatechuate-3,4-Dioxygenase Proteins 0.000 description 1
- 241000489256 Pseudomonas aeruginosa PA7 Species 0.000 description 1
- 241001240958 Pseudomonas aeruginosa PAO1 Species 0.000 description 1
- 241000948012 Pseudomonas mendocina ymp Species 0.000 description 1
- 241000589776 Pseudomonas putida Species 0.000 description 1
- 241000589774 Pseudomonas sp. Species 0.000 description 1
- 241000973064 Pseudomonas sp. SCT Species 0.000 description 1
- 101710103333 Putative monooxygenase YdhR Proteins 0.000 description 1
- 241000232299 Ralstonia Species 0.000 description 1
- 241000321184 Raoultella Species 0.000 description 1
- 102000001218 Rec A Recombinases Human genes 0.000 description 1
- 241000191025 Rhodobacter Species 0.000 description 1
- 241000190932 Rhodopseudomonas Species 0.000 description 1
- 108020001027 Ribosomal DNA Proteins 0.000 description 1
- 241001662468 Rubrobacteraceae Species 0.000 description 1
- QAXCLVRLDARCAH-UHFFFAOYSA-N SC(CCCCCC)S(=O)(=O)O Chemical compound SC(CCCCCC)S(=O)(=O)O QAXCLVRLDARCAH-UHFFFAOYSA-N 0.000 description 1
- 108091077843 SUN family Proteins 0.000 description 1
- 101100341123 Saccharomyces cerevisiae (strain ATCC 204508 / S288c) IRA2 gene Proteins 0.000 description 1
- 102100036546 Salivary acidic proline-rich phosphoprotein 1/2 Human genes 0.000 description 1
- 101800001700 Saposin-D Proteins 0.000 description 1
- 101100460203 Schizosaccharomyces pombe (strain 972 / ATCC 24843) new2 gene Proteins 0.000 description 1
- 238000012300 Sequence Analysis Methods 0.000 description 1
- 241000607720 Serratia Species 0.000 description 1
- 241000863430 Shewanella Species 0.000 description 1
- PMZURENOXWZQFD-UHFFFAOYSA-L Sodium Sulfate Chemical compound [Na+].[Na+].[O-]S([O-])(=O)=O PMZURENOXWZQFD-UHFFFAOYSA-L 0.000 description 1
- 241000589971 Spirochaetaceae Species 0.000 description 1
- 241000204388 Sporomusa Species 0.000 description 1
- 241000191940 Staphylococcus Species 0.000 description 1
- 241000191984 Staphylococcus haemolyticus Species 0.000 description 1
- 229920002472 Starch Polymers 0.000 description 1
- 229910000831 Steel Inorganic materials 0.000 description 1
- 102000019197 Superoxide Dismutase Human genes 0.000 description 1
- 108010012715 Superoxide dismutase Proteins 0.000 description 1
- 241000606017 Syntrophomonas Species 0.000 description 1
- 241001673931 Thermacetogenium phaeum Species 0.000 description 1
- 241001137870 Thermoanaerobacterium Species 0.000 description 1
- 241001133209 Thermosediminibacter Species 0.000 description 1
- JZRWCGZRTZMZEH-UHFFFAOYSA-N Thiamine Natural products CC1=C(CCO)SC=[N+]1CC1=CN=C(C)N=C1N JZRWCGZRTZMZEH-UHFFFAOYSA-N 0.000 description 1
- 241000605118 Thiobacillus Species 0.000 description 1
- 102100036407 Thioredoxin Human genes 0.000 description 1
- 241000694893 Tistrella Species 0.000 description 1
- 239000007984 Tris EDTA buffer Substances 0.000 description 1
- 101710136122 Tryptophan 2,3-dioxygenase Proteins 0.000 description 1
- 102000057288 Tryptophan 2,3-dioxygenases Human genes 0.000 description 1
- 241000607598 Vibrio Species 0.000 description 1
- 241000607343 Vibrio cholerae O1 biovar El Tor Species 0.000 description 1
- 241000272506 Vibrio parahaemolyticus RIMD 2210633 Species 0.000 description 1
- 229930003779 Vitamin B12 Natural products 0.000 description 1
- 241000605941 Wolinella Species 0.000 description 1
- PVYFQVIFEVRLRY-BLPRJPCASA-N [[(2r,3s,4r,5r)-5-(6-aminopurin-9-yl)-4-hydroxy-3-phosphonooxyoxolan-2-yl]methoxy-hydroxyphosphoryl] [(3r)-3-hydroxy-2,2-dimethyl-4-oxo-4-[[3-oxo-3-(2-sulfanylethylamino)propyl]amino]butyl] hydrogen phosphate;2-phenylacetic acid Chemical compound OC(=O)CC1=CC=CC=C1.O[C@@H]1[C@H](OP(O)(O)=O)[C@@H](COP(O)(=O)OP(O)(=O)OCC(C)(C)[C@@H](O)C(=O)NCCC(=O)NCCS)O[C@H]1N1C2=NC=NC(N)=C2N=C1 PVYFQVIFEVRLRY-BLPRJPCASA-N 0.000 description 1
- 230000006978 adaptation Effects 0.000 description 1
- 238000005273 aeration Methods 0.000 description 1
- 241001148470 aerobic bacillus Species 0.000 description 1
- 239000011543 agarose gel Substances 0.000 description 1
- 150000001298 alcohols Chemical class 0.000 description 1
- 125000001931 aliphatic group Chemical group 0.000 description 1
- 102000019199 alpha-Mannosidase Human genes 0.000 description 1
- 108010012864 alpha-Mannosidase Proteins 0.000 description 1
- 229940024606 amino acid Drugs 0.000 description 1
- 235000001014 amino acid Nutrition 0.000 description 1
- 150000001413 amino acids Chemical class 0.000 description 1
- 230000003321 amplification Effects 0.000 description 1
- 230000009604 anaerobic growth Effects 0.000 description 1
- 239000003963 antioxidant agent Substances 0.000 description 1
- 230000003078 antioxidant effect Effects 0.000 description 1
- 235000006708 antioxidants Nutrition 0.000 description 1
- GCPXMJHSNVMWNM-UHFFFAOYSA-N arsenous acid Chemical class O[As](O)O GCPXMJHSNVMWNM-UHFFFAOYSA-N 0.000 description 1
- 102000028848 arylesterase Human genes 0.000 description 1
- 108010009043 arylesterase Proteins 0.000 description 1
- 235000010323 ascorbic acid Nutrition 0.000 description 1
- 229960005070 ascorbic acid Drugs 0.000 description 1
- 239000011668 ascorbic acid Substances 0.000 description 1
- 235000010233 benzoic acid Nutrition 0.000 description 1
- 108010051210 beta-Fructofuranosidase Proteins 0.000 description 1
- 108010047754 beta-Glucosidase Proteins 0.000 description 1
- 102000006995 beta-Glucosidase Human genes 0.000 description 1
- 108010085377 beta-N-Acetylhexosaminidases Proteins 0.000 description 1
- 102000007478 beta-N-Acetylhexosaminidases Human genes 0.000 description 1
- 238000006065 biodegradation reaction Methods 0.000 description 1
- 239000007956 bioemulsifier Substances 0.000 description 1
- 230000004071 biological effect Effects 0.000 description 1
- 239000012620 biological material Substances 0.000 description 1
- 230000031018 biological processes and functions Effects 0.000 description 1
- 239000000090 biomarker Substances 0.000 description 1
- 235000020958 biotin Nutrition 0.000 description 1
- 239000011616 biotin Substances 0.000 description 1
- 229960002685 biotin Drugs 0.000 description 1
- YKOQAAJBYBTSBS-UHFFFAOYSA-N biphenyl-2,3-diol Chemical compound OC1=CC=CC(C=2C=CC=CC=2)=C1O YKOQAAJBYBTSBS-UHFFFAOYSA-N 0.000 description 1
- 108010083912 bleomycin N-acetyltransferase Proteins 0.000 description 1
- OWBTYPJTUOEWEK-UHFFFAOYSA-N butane-2,3-diol Chemical compound CC(O)C(C)O OWBTYPJTUOEWEK-UHFFFAOYSA-N 0.000 description 1
- 229920005549 butyl rubber Polymers 0.000 description 1
- 229960005069 calcium Drugs 0.000 description 1
- 150000001721 carbon Chemical group 0.000 description 1
- 229910002091 carbon monoxide Inorganic materials 0.000 description 1
- 239000000969 carrier Substances 0.000 description 1
- 238000006555 catalytic reaction Methods 0.000 description 1
- 101150104736 ccsB gene Proteins 0.000 description 1
- 229940106157 cellulase Drugs 0.000 description 1
- 238000005119 centrifugation Methods 0.000 description 1
- 230000008859 change Effects 0.000 description 1
- 239000003610 charcoal Substances 0.000 description 1
- 239000003638 chemical reducing agent Substances 0.000 description 1
- 108010075269 chlorate reductase Proteins 0.000 description 1
- 108010055547 chlorite dismutase Proteins 0.000 description 1
- YTRQFSDWAXHJCC-UHFFFAOYSA-N chloroform;phenol Chemical compound ClC(Cl)Cl.OC1=CC=CC=C1 YTRQFSDWAXHJCC-UHFFFAOYSA-N 0.000 description 1
- 235000013985 cinnamic acid Nutrition 0.000 description 1
- 229930016911 cinnamic acid Natural products 0.000 description 1
- 238000004140 cleaning Methods 0.000 description 1
- 239000013599 cloning vector Substances 0.000 description 1
- 239000011248 coating agent Substances 0.000 description 1
- FDJOLVPMNUYSCM-WZHZPDAFSA-L cobalt(3+);[(2r,3s,4r,5s)-5-(5,6-dimethylbenzimidazol-1-yl)-4-hydroxy-2-(hydroxymethyl)oxolan-3-yl] [(2r)-1-[3-[(1r,2r,3r,4z,7s,9z,12s,13s,14z,17s,18s,19r)-2,13,18-tris(2-amino-2-oxoethyl)-7,12,17-tris(3-amino-3-oxopropyl)-3,5,8,8,13,15,18,19-octamethyl-2 Chemical compound [Co+3].N#[C-].N([C@@H]([C@]1(C)[N-]\C([C@H]([C@@]1(CC(N)=O)C)CCC(N)=O)=C(\C)/C1=N/C([C@H]([C@@]1(CC(N)=O)C)CCC(N)=O)=C\C1=N\C([C@H](C1(C)C)CCC(N)=O)=C/1C)[C@@H]2CC(N)=O)=C\1[C@]2(C)CCC(=O)NC[C@@H](C)OP([O-])(=O)O[C@H]1[C@@H](O)[C@@H](N2C3=CC(C)=C(C)C=C3N=C2)O[C@@H]1CO FDJOLVPMNUYSCM-WZHZPDAFSA-L 0.000 description 1
- ZNEWHQLOPFWXOF-UHFFFAOYSA-N coenzyme M Chemical compound OS(=O)(=O)CCS ZNEWHQLOPFWXOF-UHFFFAOYSA-N 0.000 description 1
- 238000010835 comparative analysis Methods 0.000 description 1
- 229910052802 copper Inorganic materials 0.000 description 1
- 108010058646 cyclohexanone oxygenase Proteins 0.000 description 1
- 229940104302 cytosine Drugs 0.000 description 1
- 238000006731 degradation reaction Methods 0.000 description 1
- 230000018044 dehydration Effects 0.000 description 1
- 238000006297 dehydration reaction Methods 0.000 description 1
- 230000017858 demethylation Effects 0.000 description 1
- 238000010520 demethylation reaction Methods 0.000 description 1
- 230000001419 dependent effect Effects 0.000 description 1
- 108010049285 dephospho-CoA kinase Proteins 0.000 description 1
- 238000001514 detection method Methods 0.000 description 1
- 238000010790 dilution Methods 0.000 description 1
- 239000012895 dilution Substances 0.000 description 1
- 238000006471 dimerization reaction Methods 0.000 description 1
- 229910001882 dioxygen Inorganic materials 0.000 description 1
- 238000009826 distribution Methods 0.000 description 1
- 239000003814 drug Substances 0.000 description 1
- 238000004520 electroporation Methods 0.000 description 1
- 238000005516 engineering process Methods 0.000 description 1
- 108010005535 ethylbenzene dehydrogenase Proteins 0.000 description 1
- 108010055265 exo-1,6-alpha-glucosidase Proteins 0.000 description 1
- 239000003337 fertilizer Substances 0.000 description 1
- 238000001914 filtration Methods 0.000 description 1
- 229960000304 folic acid Drugs 0.000 description 1
- 235000019152 folic acid Nutrition 0.000 description 1
- 239000011724 folic acid Substances 0.000 description 1
- 238000009472 formulation Methods 0.000 description 1
- 238000013467 fragmentation Methods 0.000 description 1
- 238000006062 fragmentation reaction Methods 0.000 description 1
- 238000010230 functional analysis Methods 0.000 description 1
- 230000002538 fungal effect Effects 0.000 description 1
- 238000001502 gel electrophoresis Methods 0.000 description 1
- 235000003869 genetically modified organism Nutrition 0.000 description 1
- 239000008103 glucose Substances 0.000 description 1
- 108010050669 glucosidase I Proteins 0.000 description 1
- 239000003673 groundwater Substances 0.000 description 1
- 239000003102 growth factor Substances 0.000 description 1
- 239000000665 guar gum Substances 0.000 description 1
- 235000010417 guar gum Nutrition 0.000 description 1
- 229960002154 guar gum Drugs 0.000 description 1
- 229940093915 gynecological organic acid Drugs 0.000 description 1
- 238000010438 heat treatment Methods 0.000 description 1
- 230000003403 homoacetogenic effect Effects 0.000 description 1
- 235000003642 hunger Nutrition 0.000 description 1
- 229960002773 hyaluronidase Drugs 0.000 description 1
- BHEPBYXIRTUNPN-UHFFFAOYSA-N hydridophosphorus(.) (triplet) Chemical class [PH] BHEPBYXIRTUNPN-UHFFFAOYSA-N 0.000 description 1
- 125000004435 hydrogen atom Chemical group [H]* 0.000 description 1
- 238000010348 incorporation Methods 0.000 description 1
- 230000003993 interaction Effects 0.000 description 1
- 239000001573 invertase Substances 0.000 description 1
- 235000011073 invertase Nutrition 0.000 description 1
- 238000011835 investigation Methods 0.000 description 1
- 238000009533 lab test Methods 0.000 description 1
- 239000004310 lactic acid Substances 0.000 description 1
- 235000014655 lactic acid Nutrition 0.000 description 1
- 229920005610 lignin Polymers 0.000 description 1
- 230000001533 ligninolytic effect Effects 0.000 description 1
- AGBQKNBQESQNJD-UHFFFAOYSA-M lipoate Chemical compound [O-]C(=O)CCCCC1CCSS1 AGBQKNBQESQNJD-UHFFFAOYSA-M 0.000 description 1
- 235000019136 lipoic acid Nutrition 0.000 description 1
- 230000004807 localization Effects 0.000 description 1
- 230000007774 longterm Effects 0.000 description 1
- 239000011777 magnesium Substances 0.000 description 1
- 229910052749 magnesium Inorganic materials 0.000 description 1
- 239000011159 matrix material Substances 0.000 description 1
- 238000011177 media preparation Methods 0.000 description 1
- 108010009977 methane monooxygenase Proteins 0.000 description 1
- WBYWAXJHAXSJNI-UHFFFAOYSA-N methyl p-hydroxycinnamate Natural products OC(=O)C=CC1=CC=CC=C1 WBYWAXJHAXSJNI-UHFFFAOYSA-N 0.000 description 1
- FGMRHOCVEPGURB-UHFFFAOYSA-N methyl-CoM Chemical compound CSCCS(O)(=O)=O FGMRHOCVEPGURB-UHFFFAOYSA-N 0.000 description 1
- 150000003956 methylamines Chemical class 0.000 description 1
- 230000007269 microbial metabolism Effects 0.000 description 1
- 238000009629 microbiological culture Methods 0.000 description 1
- 238000000386 microscopy Methods 0.000 description 1
- 238000005065 mining Methods 0.000 description 1
- 238000002156 mixing Methods 0.000 description 1
- 239000003607 modifier Substances 0.000 description 1
- 229910052750 molybdenum Inorganic materials 0.000 description 1
- 238000002887 multiple sequence alignment Methods 0.000 description 1
- 229910052759 nickel Inorganic materials 0.000 description 1
- 235000001968 nicotinic acid Nutrition 0.000 description 1
- 229960003512 nicotinic acid Drugs 0.000 description 1
- 239000011664 nicotinic acid Substances 0.000 description 1
- 238000003199 nucleic acid amplification method Methods 0.000 description 1
- 238000007826 nucleic acid assay Methods 0.000 description 1
- 239000002773 nucleotide Substances 0.000 description 1
- 125000003729 nucleotide group Chemical group 0.000 description 1
- 238000005457 optimization Methods 0.000 description 1
- 235000005985 organic acids Nutrition 0.000 description 1
- 230000000972 organotrophic effect Effects 0.000 description 1
- 238000007248 oxidative elimination reaction Methods 0.000 description 1
- 230000036542 oxidative stress Effects 0.000 description 1
- QVGXLLKOCUKJST-NJFSPNSNSA-N oxygen-18 atom Chemical compound [18O] QVGXLLKOCUKJST-NJFSPNSNSA-N 0.000 description 1
- LPNBBFKOUUSUDB-UHFFFAOYSA-N p-toluic acid Chemical compound CC1=CC=C(C(O)=O)C=C1 LPNBBFKOUUSUDB-UHFFFAOYSA-N 0.000 description 1
- 229940014662 pantothenate Drugs 0.000 description 1
- 235000019161 pantothenic acid Nutrition 0.000 description 1
- 239000011713 pantothenic acid Substances 0.000 description 1
- VLTRZXGMWDSKGL-UHFFFAOYSA-M perchlorate Inorganic materials [O-]Cl(=O)(=O)=O VLTRZXGMWDSKGL-UHFFFAOYSA-M 0.000 description 1
- VLTRZXGMWDSKGL-UHFFFAOYSA-N perchloric acid Chemical compound OCl(=O)(=O)=O VLTRZXGMWDSKGL-UHFFFAOYSA-N 0.000 description 1
- 239000003208 petroleum Substances 0.000 description 1
- 239000003209 petroleum derivative Substances 0.000 description 1
- CMPQUABWPXYYSH-UHFFFAOYSA-N phenyl phosphate Chemical compound OP(O)(=O)OC1=CC=CC=C1 CMPQUABWPXYYSH-UHFFFAOYSA-N 0.000 description 1
- 150000003018 phosphorus compounds Chemical class 0.000 description 1
- 125000003367 polycyclic group Chemical group 0.000 description 1
- 229920001223 polyethylene glycol Polymers 0.000 description 1
- 235000019446 polyethylene glycol 8000 Nutrition 0.000 description 1
- 229940085678 polyethylene glycol 8000 Drugs 0.000 description 1
- 108010045801 polysaccharide deacetylase Proteins 0.000 description 1
- 239000001267 polyvinylpyrrolidone Substances 0.000 description 1
- 235000013855 polyvinylpyrrolidone Nutrition 0.000 description 1
- 229920000036 polyvinylpyrrolidone Polymers 0.000 description 1
- 239000011148 porous material Substances 0.000 description 1
- 238000002360 preparation method Methods 0.000 description 1
- 238000002203 pretreatment Methods 0.000 description 1
- 238000012545 processing Methods 0.000 description 1
- 229960000856 protein c Drugs 0.000 description 1
- 238000010188 recombinant method Methods 0.000 description 1
- 230000001105 regulatory effect Effects 0.000 description 1
- 238000011160 research Methods 0.000 description 1
- 235000019192 riboflavin Nutrition 0.000 description 1
- 229960002477 riboflavin Drugs 0.000 description 1
- 239000002151 riboflavin Substances 0.000 description 1
- 238000003385 ring cleavage reaction Methods 0.000 description 1
- 108060007223 rubredoxin Proteins 0.000 description 1
- 230000001523 saccharolytic effect Effects 0.000 description 1
- 230000028327 secretion Effects 0.000 description 1
- 239000005421 sedimentary organic matter Substances 0.000 description 1
- 238000004062 sedimentation Methods 0.000 description 1
- 210000002966 serum Anatomy 0.000 description 1
- 239000010454 slate Substances 0.000 description 1
- 229910052708 sodium Inorganic materials 0.000 description 1
- 235000010344 sodium nitrate Nutrition 0.000 description 1
- 239000004317 sodium nitrate Substances 0.000 description 1
- 229910052938 sodium sulfate Inorganic materials 0.000 description 1
- 229910052979 sodium sulfide Inorganic materials 0.000 description 1
- GRVFOGOEDUUMBP-UHFFFAOYSA-N sodium sulfide (anhydrous) Chemical compound [Na+].[Na+].[S-2] GRVFOGOEDUUMBP-UHFFFAOYSA-N 0.000 description 1
- 235000011152 sodium sulphate Nutrition 0.000 description 1
- 238000004611 spectroscopical analysis Methods 0.000 description 1
- 229940063673 spermidine Drugs 0.000 description 1
- 229910001220 stainless steel Inorganic materials 0.000 description 1
- 239000010935 stainless steel Substances 0.000 description 1
- 229940037649 staphylococcus haemolyticus Drugs 0.000 description 1
- 235000019698 starch Nutrition 0.000 description 1
- 239000008107 starch Substances 0.000 description 1
- 230000037351 starvation Effects 0.000 description 1
- 239000010959 steel Substances 0.000 description 1
- 235000000346 sugar Nutrition 0.000 description 1
- 239000013589 supplement Substances 0.000 description 1
- 239000002352 surface water Substances 0.000 description 1
- 230000002459 sustained effect Effects 0.000 description 1
- 238000013268 sustained release Methods 0.000 description 1
- 239000012730 sustained-release form Substances 0.000 description 1
- 238000003786 synthesis reaction Methods 0.000 description 1
- 238000010189 synthetic method Methods 0.000 description 1
- 230000009897 systematic effect Effects 0.000 description 1
- 229960003080 taurine Drugs 0.000 description 1
- 238000004227 thermal cracking Methods 0.000 description 1
- 230000000476 thermogenic effect Effects 0.000 description 1
- KYMBYSLLVAOCFI-UHFFFAOYSA-N thiamine Chemical compound CC1=C(CCO)SCN1CC1=CN=C(C)N=C1N KYMBYSLLVAOCFI-UHFFFAOYSA-N 0.000 description 1
- 229960003495 thiamine Drugs 0.000 description 1
- 235000019157 thiamine Nutrition 0.000 description 1
- 239000011721 thiamine Substances 0.000 description 1
- 229960002663 thioctic acid Drugs 0.000 description 1
- 150000003568 thioethers Chemical class 0.000 description 1
- 108060008226 thioredoxin Proteins 0.000 description 1
- 229940094937 thioredoxin Drugs 0.000 description 1
- 108010005809 toluene-4-monooxygenase Proteins 0.000 description 1
- 238000012546 transfer Methods 0.000 description 1
- 238000000844 transformation Methods 0.000 description 1
- 230000032258 transport Effects 0.000 description 1
- 238000005829 trimerization reaction Methods 0.000 description 1
- 241001099134 unclassified Bacillus Species 0.000 description 1
- 241000344485 unclassified Bacteroidales Species 0.000 description 1
- 241001423434 unclassified Enterobacteriaceae Species 0.000 description 1
- 241001277910 unclassified Rhodocyclaceae Species 0.000 description 1
- 241000043010 unclassified Rikenellaceae Species 0.000 description 1
- 241000131979 unclassified Sphingomonadaceae Species 0.000 description 1
- 241001423442 unclassified Xanthomonadaceae Species 0.000 description 1
- 241001300301 uncultured bacterium Species 0.000 description 1
- WKOLLVMJNQIZCI-UHFFFAOYSA-M vanillate Chemical compound COC1=CC(C([O-])=O)=CC=C1O WKOLLVMJNQIZCI-UHFFFAOYSA-M 0.000 description 1
- 239000013598 vector Substances 0.000 description 1
- 230000035899 viability Effects 0.000 description 1
- 235000019163 vitamin B12 Nutrition 0.000 description 1
- 239000011715 vitamin B12 Substances 0.000 description 1
- 150000003722 vitamin derivatives Chemical class 0.000 description 1
- 235000019195 vitamin supplement Nutrition 0.000 description 1
- 238000005406 washing Methods 0.000 description 1
- 229910052725 zinc Inorganic materials 0.000 description 1
- DGVVWUTYPXICAM-UHFFFAOYSA-N β‐Mercaptoethanol Chemical compound OCCS DGVVWUTYPXICAM-UHFFFAOYSA-N 0.000 description 1
Images
Classifications
-
- E—FIXED CONSTRUCTIONS
- E21—EARTH OR ROCK DRILLING; MINING
- E21B—EARTH OR ROCK DRILLING; OBTAINING OIL, GAS, WATER, SOLUBLE OR MELTABLE MATERIALS OR A SLURRY OF MINERALS FROM WELLS
- E21B43/00—Methods or apparatus for obtaining oil, gas, water, soluble or meltable materials or a slurry of minerals from wells
- E21B43/006—Production of coal-bed methane
-
- C—CHEMISTRY; METALLURGY
- C09—DYES; PAINTS; POLISHES; NATURAL RESINS; ADHESIVES; COMPOSITIONS NOT OTHERWISE PROVIDED FOR; APPLICATIONS OF MATERIALS NOT OTHERWISE PROVIDED FOR
- C09K—MATERIALS FOR MISCELLANEOUS APPLICATIONS, NOT PROVIDED FOR ELSEWHERE
- C09K8/00—Compositions for drilling of boreholes or wells; Compositions for treating boreholes or wells, e.g. for completion or for remedial operations
- C09K8/58—Compositions for enhanced recovery methods for obtaining hydrocarbons, i.e. for improving the mobility of the oil, e.g. displacing fluids
- C09K8/582—Compositions for enhanced recovery methods for obtaining hydrocarbons, i.e. for improving the mobility of the oil, e.g. displacing fluids characterised by the use of bacteria
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N1/00—Microorganisms, e.g. protozoa; Compositions thereof; Processes of propagating, maintaining or preserving microorganisms or compositions thereof; Processes of preparing or isolating a composition containing a microorganism; Culture media therefor
- C12N1/20—Bacteria; Culture media therefor
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12P—FERMENTATION OR ENZYME-USING PROCESSES TO SYNTHESISE A DESIRED CHEMICAL COMPOUND OR COMPOSITION OR TO SEPARATE OPTICAL ISOMERS FROM A RACEMIC MIXTURE
- C12P5/00—Preparation of hydrocarbons or halogenated hydrocarbons
- C12P5/02—Preparation of hydrocarbons or halogenated hydrocarbons acyclic
- C12P5/023—Methane
-
- Y—GENERAL TAGGING OF NEW TECHNOLOGICAL DEVELOPMENTS; GENERAL TAGGING OF CROSS-SECTIONAL TECHNOLOGIES SPANNING OVER SEVERAL SECTIONS OF THE IPC; TECHNICAL SUBJECTS COVERED BY FORMER USPC CROSS-REFERENCE ART COLLECTIONS [XRACs] AND DIGESTS
- Y02—TECHNOLOGIES OR APPLICATIONS FOR MITIGATION OR ADAPTATION AGAINST CLIMATE CHANGE
- Y02E—REDUCTION OF GREENHOUSE GAS [GHG] EMISSIONS, RELATED TO ENERGY GENERATION, TRANSMISSION OR DISTRIBUTION
- Y02E50/00—Technologies for the production of fuel of non-fossil origin
- Y02E50/30—Fuel from waste, e.g. synthetic alcohol or diesel
Landscapes
- Chemical & Material Sciences (AREA)
- Engineering & Computer Science (AREA)
- Life Sciences & Earth Sciences (AREA)
- Organic Chemistry (AREA)
- Wood Science & Technology (AREA)
- Health & Medical Sciences (AREA)
- Zoology (AREA)
- Genetics & Genomics (AREA)
- Bioinformatics & Cheminformatics (AREA)
- Biotechnology (AREA)
- General Engineering & Computer Science (AREA)
- Geology (AREA)
- General Chemical & Material Sciences (AREA)
- Chemical Kinetics & Catalysis (AREA)
- Biochemistry (AREA)
- Mining & Mineral Resources (AREA)
- General Life Sciences & Earth Sciences (AREA)
- General Health & Medical Sciences (AREA)
- Oil, Petroleum & Natural Gas (AREA)
- Microbiology (AREA)
- Medicinal Chemistry (AREA)
- Virology (AREA)
- Biomedical Technology (AREA)
- Physics & Mathematics (AREA)
- Environmental & Geological Engineering (AREA)
- Fluid Mechanics (AREA)
- Tropical Medicine & Parasitology (AREA)
- Materials Engineering (AREA)
- Geochemistry & Mineralogy (AREA)
- Micro-Organisms Or Cultivation Processes Thereof (AREA)
- Preparation Of Compounds By Using Micro-Organisms (AREA)
- Measuring Or Testing Involving Enzymes Or Micro-Organisms (AREA)
- Organic Low-Molecular-Weight Compounds And Preparation Thereof (AREA)
Abstract
Изобретение относится к области биотехнологии и может быть использовано для повышения биогенного продуцирования метана. Способ включает: (a) получение последовательности нуклеиновой кислоты от одного или более микроорганизмов, выделенных из среды углеводородсодержащего пласта; (b) определение присутствия одного или более генных продуктов указанной последовательности нуклеиновой кислоты, где указанный генный продукт представляет собой фермент на пути метаболизма, вовлеченного в преобразование углеводорода в метан, выбранный из группы, состоящей из пероксидаз, фенолоксидаз, алкогольоксидаз, лакказ, гидролаз, гликозилгидролаз, эстераз, этераз, оксидаз, нитрогеназ, целлюлаз, амилаз, глюканаз, пуллуланаз, редуктаз, дисмутаз, оксигеназ, монооксигеназ, диоксигеназ, каталаз, гидрогеназ, карбоксилаз и метилредуктаз; или фермент, вовлеченный в гомоацетогенез, метаногенез, ацетокластический метаногенез или CO-восстановительный метаногенез; и (c) идентификацию субстрата, реактанта или кофактора указанного фермента, который повышает продуцирование метана, будучи доступным одному или более микроорганизмам в указанном углеводородсодержащем пласте, и (d) идентификация тем самым стимулятора, который повышает биогенное продуцирование метана в углеводородсодержащем пласте по сравнению с продуцированием метана в углеводородсодержащем пласте в отсутствие стимулятора. Изобретение позволяет эффективно стимулировать биогенное продуцирование метана в углеводородсодержащих пластах. 4 н. и 11 з.п. ф-лы, 16 ил., 3 табл., 3 пр.
Description
Перекрестная ссылка на родственную заявку
По настоящей заявке испрашивается приоритет согласно предварительной заявке США № 61/052624, поданной 12 мая 2008 года, которая включена в настоящее описание посредством ссылки во всей своей полноте.
Уровень техники
Настоящее изобретение в основном относится к молекулярной характеристике автохтонных метан-продуцирующих микроорганизмов и их определенных сообществ из углеводородсодержащих пластов, таких как угольные пласты; и более конкретно, к анализам геномных данных окружающей среды из таких микроорганизмов и применению таких данных и микроорганизмов для увеличения степени конверсии и извлечения метана с использованием стимуляторов, идентифицированных путем определения присутствия ферментов в метаболических путях, участвующих в конверсии углеводорода в метан.
Метан угольных пластов (CBM) является источником природного газа, образующегося либо биологически, либо термогенно в угольных месторождениях. Биогенное продуцирование CBM является результатом микробного метаболизма и разложения угля с последующим обменом электронами между многочисленными микробными популяциями. Термогенное продуцирование CBM является результатом термического крекинга осадочного органического вещества или нефти, происходящего позже при углефикации, когда температуры поднимаются выше уровней, при которых могут существовать метан-продуцирующие микроорганизмы. В угольных пластах давление вышележащих горных пород и окружающей воды вынуждает CBM связываться с поверхностью угля и абсорбироваться в твердую матрицу угля в виде свободного газа в микропорах и зонах кливажа (расщепление угольной породы сетью трещин на тонкие пластины и т.д.), в виде растворенного в воде газа, в виде адсорбированного газа, удерживаемого силами молекулярного притяжения на поверхности мацералов (органических составляющих, которые образуют угольную массу), микропор и зон кливажа в угле, и в виде газа, абсорбированного внутри молекулярной структуры угля.
Уголь представляет собой осадочную породу c различными степенями проницаемости, причем метан находится преимущественно в зонах кливажа. Эти трещины в угле действуют в качестве основных каналов, обеспечивающих возможность течения CBM. Для извлечения CBM в угольном пласте бурят скважину со стальной обсадной колонной, которая дает возможность снизить давление благодаря выходу скважины на поверхность или откачивать небольшое количество воды из угольного пласта (обезвоживание). CBM имеет очень низкую растворимость в воде и легко выделяется при снижении давления, что дает возможность откачивать его из скважины отдельно от воды. Затем CBM поступает в компрессорную станцию и в трубопроводы для природного газа.
CBM составляет значительную часть природного газа, добываемого в США, обеспечивая, по оценкам, приблизительно 10% поставок природного газа, или примерно 1,8 триллиона кубических футов (TCF) (50 миллиардов кубических метров). Международные ресурсы обеспечивают огромные возможности добычи CBM в будущем. К наиболее продуктивным областям относится бассейн Сан-Хуан (San Juan), расположенный в Колорадо и Нью-Мексико. При наличии таких огромных месторождений CBM минимальные улучшения степени извлечения CBM могут, таким образом, привести к значительному увеличению добычи из скважины, и в соответствии с этим разрабатываются различные способы для улучшения степени извлечения CBM из угольных пластов.
Чисто физические воздействия могут включать оптимизацию способов бурения и разрыва пласта. Другие способы усовершенствования включают воздействие внешних факторов непосредственно на угольные пласты. Они включают, например, нагнетание газов, таких как азот (см., например, Shimizu, S., Akiyama, M., Naganuma, T., Fujioka, M., Nako M. и Ishijima, Y. 2007. Molecular characterization of microbial communities in deep coal seam groundwater of northern Japan. Geobiology, 5(4): 423-433; патент США 4883122) и CO2 (см., например, патент США 5402847); и закачивание горячих текучих сред, таких как вода или пар (см., например, патент США 5072990). Различные способы предназначены для увеличения проницаемости угольных пластов либо физическими (см., например, патент США 5014788), либо химическими (см., например, патент США 5865248) методами.
Впоследствии разрабатывались усовершенствованные способы стимуляции биогенного продуцирования метана в существующих скважинах. В патенте США 5424195 раскрыто использование консорции микроорганизмов, культивируемых in situ или на содержащем уголь субстрате, для биологического превращения угля в метан. В PCT/GB2006/004443 (WO2007/060473) представлены способы получения и применения культуры подземных микроорганизмов. В PCT/US2006/039352 (WO2008/041990) раскрыты способы и системы для стимуляции биогенного продуцирования путем нагнетания закачиваемой текучей среды, которая способствует анаэробному биологическому разложению нежидких углеводородов в пласте автохтонными микроорганизмами. В PCT/US2007/080161 (WO2008/042888) раскрыты способы, включающие нагревание in situ пласта с нежидкими углеводородами для обеспечения биогенного продуцирования метана. В патенте США 7426960 раскрыты способы стимуляции биогенного продуцирования метаболита с повышенным содержанием водорода, включающие закачивание воды в выработку для распределения в ней консорции микроорганизмов. В патенте США 6543535 раскрыты способы стимуляции активности микробных сообществ в углеводородсодержащем подземном пласте для превращения углеводородов в метан с использованием информации, полученной в результате анализа компонентов пласта и характеризации микроорганизмов в консорциях. Хотя в патенте США 6543535 предусмотрено сравнение выделенных микроорганизмов с известными микроорганизмами, для установления филогенетической идентичности таким известным организмам, в нем не раскрыта идентификация или использование специфических генов, кодирующих ферменты, которые участвуют в биотрансформации угля в метан, из метанобразующих бактерий в пределах сообществ, или использование анализа активности ферментов для выявления новых стимуляторов. В публикации патентной заявки США № 2008/0289816 раскрыты способы введения микроорганизмов в углеродсодержащий материал в анаэробной среде и увеличения биогенного продуцирования углеводородов, включающие использование модифицированных пластовых вод. В публикации патентной заявки США № 2008/0299635 раскрыты способы стимуляции продуцирования метана из углеродного материала с метаногенной консорцией. В публикации патентной заявки США № 2009/0023612 раскрыты способы увеличения биогенного продуцирования горючего газа из углеродного материала, предусматривающие использование анаэробного сообщества, включающего виды Pseudomonas. В публикации патентной заявки США № 2009/0023611 раскрыты изолированные микробные сообщества для биогенного продуцирования метана из сложных углеводородов, включающие виды Thermotoga. В публикации патентной заявки США № 2008/0286855 раскрыт способ увеличения продуцирования материалов с повышенным содержанием водорода, включающий введение сообщества, содержащего выделенную культуру Thermacetogenium phaeum. В патенте США № 7416879 раскрыты способы стимуляции биологической активности Thermacetogenium phaeum в геологическом пласте, включающие введение в пласт модификатора. В публикации патентной заявки США № 2008/0182318 раскрыты выделенные микробные сообщества для биогенного продуцирования метана, содержащие виды Desulfuromonas. В публикации патентной заявки США № 2007/0295505 раскрыты способы стимуляции биогенного продуцирования продукта метаболизма с повышенным содержанием водорода в геологическом пласте, который включает углеродный материал, включающие обеспечение фосфорного соединения для присутствующих в них микроорганизмов. В публикации патентной заявки США № 2007/0261843 раскрыты способы стимуляции биогенного продуцирования продукта метаболизма с повышенным содержанием водорода в геологическом пласте, который включает углеродный материал, включающие обеспечение доступности соединений водорода и фосфора для присутствующих в них микроорганизмов. В PCT/US2006/031723 (WO2007/022122) раскрыты системы для усиления биогенного продуцирования метана, включающие модифицирующую CBM воду и другие содержащие микроорганизмы среды, уменьшающие конкуренцию за восстановление сульфатов и увеличивающие концентрацию органических веществ.
Биогенное продуцирование метана является результатом многочисленных возможных ферментативных путей метаболизма, которые последовательно разрушают комплексные макромолекулярные полициклические органические вещества, образующиеся из лигнина. Например, лигнинолитические ферменты могут включать пероксидазы (марганецпероксидаза, лигнинпероксидазы и т.д.), фенолоксидазы (лакказы), гидролазы, эстеразы и оксидазы (см., например, Fakoussa, R.M. и Hofrichter, M. 1999. Biotechnology and Microbiology of Coal Degradation. Appl. Microbiol. Biotechnol. 52:25-40). Когда происходит первичная фрагментация, в реакцию начинают вступать ферменты, участвующие в деметилировании и раскрытии кольца, окислении ароматических и алифатических фрагментов и последующих метаболических путях ферментации и метаногенеза. Считается, что микроорганизмы, обитающие в углеводородсодержащих пластах, включая метан-продуцирующие бактерии, являются облигатными анаэробами.
В данной области остается потребность в эффективной стимуляции биогенного продуцирования в углеводородсодержащих пластах, таких как угольные, и в повышении производительности по CBM существующих скважин. Настоящее изобретение предлагает способы не только для идентификации и применения микроорганизмов, обитающих в окружающей среде пласта, но и для идентификации точно приспособленных воздействий (таких как стимуляторы, которые могут быть введены в окружающую среду для усиления биогенного продуцирования метана) после установления присутствия специфических генных продуктов, принимающих участие в путях метаболизма, приводящих к образованию метана.
Сущность изобретения
Настоящее изобретение предоставляет методы и способы идентификации и применения стимуляторов и ферментов для биогенного продуцирования метана в углеводородсодержащих пластах. Способы по настоящему изобретению включают использование информации о нуклеиновых кислотах, полученной от многочисленных микроорганизмов, идентифицированных в углеводородсодержащем пласте, для идентификации генных продуктов, которые представляют собой ферменты, присутствующие в микроорганизмах, которые могут функционировать в различных путях метаболизма, начиная от источника углеводорода и приводя к образованию метана. См., например, фиг.1.
В первом аспекте изобретение предоставляет способы идентификации стимулятора, который увеличивает биогенное продуцирование метана в углеводородсодержащем пласте, включающие: (а) получение последовательности нуклеиновой кислоты из одного или нескольких микроорганизмов, выделенных из среды углеводородсодержащего пласта; (b) определение присутствия одного или нескольких генных продуктов указанной последовательности нуклеиновой кислоты, где генный продукт является ферментом метаболического пути, вовлеченного в конверсию углеводорода в метан; и (с) идентификацию субстрата, реактанта или кофактора указанного фермента, который увеличивает продуцирование метана, будучи доступным для одного или нескольких микроорганизмов в указанном углеводородсодержащем пласте.
В одном варианте осуществления один или несколько микроорганизмов из углеводородсодержащего пласта улучшают путем отбора по способности к росту на угле в качестве единственном источнике углерода.
В еще одном варианте осуществления указанная выше стадия (с) включает тестирование in vitro одного или нескольких субстратов, реактантов или кофакторов при более чем одной концентрации для мониторинга и оптимизации продуцирования метана в системе культур, включающей по меньшей мере один микроорганизм, выделенный из указанного углеводородсодержащего пласта, где дополнительно для указанной системы культур уголь является единственным источником углерода.
В одном предпочтительном варианте осуществления по меньшей мере один микроорганизм представляет собой бактериальный вид или архебактериальный вид, способный преобразовывать углеводород в продукт, выбранный из группы, состоящей из водорода, диоксида углерода, ацетата, формиата, метанола, метиламина и метаногенного субстрата; вид разлагающих углеводороды бактерий, вид метаногенных бактерий или метаногенный архебактериальный вид. В еще одном предпочтительном варианте осуществления такой микроорганизм представляет собой вид бактерий, выбранных из группы родов, состоящей из Pseudomonas, Arcobacter, Desulfuromonas, Pelobacter, Desulfovibrio, Spirochaeta, Erysipelothrix, Thauera, Clostridium, Acholeplasma, Magnetospirillum и Sulfurospirillum; или вид архебактерий, выбранных из группы, состоящей из Methanolobus, Methanocalculus и членов типа Crenarcheaota.
В альтернативном варианте осуществления стадию (с) выполняют с использованием определенного микробного сообщества, которое объединяет культуру единичного штамма микроорганизма из углеводородсодержащего пласта по меньшей мере с одной другой определенной культурой еще одного единичного штамма микроорганизма так, что члены указанного определенного микробного сообщества проявляют синергическое действие в продуцировании метана; и, дополнительно, где для указанной системы культур уголь является единственным источником углерода. Предпочтительное определенное микробное сообщество включает по меньшей мере два вида микроорганизмов, выбранных из группы родов, состоящей из Pseudomonas, Arcobacter, Desulfuromonas, Pelobacter, Desulfovibrio, Spirochaeta, Erysipelothrix, Thauera, Clostridium, Acholeplasma, Magnetospirillum, Sulfurospirillum; Methanolobus, Methanocalculus и членов типа Crenarcheaota.
В различных вариантах осуществления углеводородсодержащий пласт выбирают из группы, состоящей из угля, торфа, бурого угля, битуминозного сланца, нефтеносного пласта, традиционных тяжелых нефтяных остатков, вязкой нефти, нефтеносных песков и битуминозных песков. В предпочтительном варианте осуществления пласт представляет собой уголь в угольном пласте или угольной залежи.
В различных вариантах осуществления фермент, вовлеченный в конверсию углеводорода в метан, выбирают из группы, состоящей из пероксидаз, фенолоксидаз, алкогольоксидаз, лакказ, гидролаз, гликозилгидролаз, эстераз, этераз, оксидаз, нитрогеназ, целлюлаз, амилаз, глюканаз, пулланаз, редуктаз, дисмутаз, оксигеназ, монооксигеназ, диоксигеназ, каталаз, гидрогеназ и карбоксилаз. В предпочтительном варианте осуществления фермент выбирают из группы, состоящей из оксигеназ, монооксигеназ и диоксигеназ.
В различных вариантах осуществления субстрат, реактант или кофактор выбирают из группы, состоящей из серосодержащего соединения, азотсодержащего соединения, фосфорсодержащего соединения, микроэлемента, электроноакцептора, электронодонора, галогена, металла, спирта, органической кислоты, алкана, алкена, алкина, ароматического соединения, амина, простого эфира, альдегида, кетона, тиола, ацетата, ароматического углеводорода и газа. В предпочтительном варианте осуществления реактантом является кислород.
Во втором аспекте изобретение предоставляет способы увеличения биогенного продуцирования метана в углеводородсодержащем пласте, где указанный способ включает введение в углеводородсодержащий пласт стимулятора, идентифицированного любым из описанных выше способов согласно первому аспекту.
В одном варианте осуществления способ предусматривает введение кислорода в указанный углеводородсодержащий пласт. В предпочтительном варианте осуществления углеводородсодержащий пласт представляет собой уголь.
В третьем аспекте изобретение предоставляет способы увеличения биогенного продуцирования метана в углеводородсодержащем пласте, где указанный способ включает модуляцию фермента, выбранного из группы, состоящей из пероксидаз, фенолоксидаз, алкогольоксидаз, лакказ, гидролаз, гликозилгидролаз, эстераз, этераз, оксидаз, нитрогеназ, целлюлаз, амилаз, глюканаз, пулланаз, редуктаз, дисмутаз, оксигеназ, монооксигеназ, диоксигеназ, каталаз, гидрогеназ и карбоксилаз.
В альтернативных вариантах осуществления фермент присутствует в существующем в углеводородсодержащем пласте микроорганизме, или его вводят в углеводородсодержащий пласт. В последнем варианте осуществления фермент вводят в указанный углеводородсодержащий пласт внесением микроорганизма, экспрессирующего указанный фермент. В одном варианте осуществления вводимый микроорганизм, экспрессирующий указанный фермент, представляет собой рекомбинантный микроорганизм, полученный путем модифицирования микроорганизма, выделенного из указанного углеводородсодержащего пласта. В еще одном варианте осуществления микроорганизм, экспрессирующий указанный фермент, представляет собой искусственный микроорганизм.
В четвертом аспекте изобретение предоставляет способы идентификации определенного микробного сообщества для конверсии угля в метан, включающий: (а) получение последовательности нуклеиновой кислоты из одного или нескольких микроорганизмов, выделенных из среды угля; (b) определение присутствия одного или нескольких генных продуктов указанной последовательности нуклеиновой кислоты, где указанный генный продукт является ферментом метаболического пути, вовлеченного в конверсию угля в метан; (с) получение культуры единичного штамма указанного одного или нескольких микроорганизмов из указанной среды угля, где единичный штамм микроорганизма содержит указанные один или несколько генных продуктов; и (d) объединение указанного культивированного единичного штамма микроорганизма по меньшей мере с одной другой определенной культурой еще одного единичного штамма микроорганизма, для создания определенного микробного сообщества; где члены указанного определенного микробного сообщества проявляют синергическое действие в продуцировании метана.
В одном варианте осуществления создают определенное микробное сообщество для конверсии угля в метан, идентифицированное описанными выше способами согласно изобретению.
В еще одном варианте осуществления способ дополнительно включает (е) обеспечение указанному определенному микробному сообществу, которое увеличивает продуцирование метана, доступа к субстрату, реактанту или кофактору.
В предпочтительных вариантах осуществления определенное микробное сообщество включает по меньшей мере два вида микроорганизмов, выбранных из группы родов, состоящей из Pseudomonas, Arcobacter, Desulfuromonas, Pelobacter, Desulfovibrio, Spirochaeta, Erysipelothrix, Thauera, Clostridium, Acholeplasma, Magnetospirillum, Sulfurospirillum; Methanolobus, Methanocalculus и членов типа Crenarcheaota.
В пятом аспекте изобретение предоставляет способы увеличения биогенного продуцирования метана из угля путем введения в угольный пласт определенного микробного сообщества, идентифицированного описанными в данном описании способами согласно изобретению.
В предпочтительном варианте осуществления такие способы включают введение определенного микробного сообщества, идентифицированного, как указано выше, в угольный пласт вместе с указанным субстратом, реактантом или кофактором.
Краткое описание чертежей
Фиг.1 иллюстрирует многообразие потенциальных ферментативных путей метаболизма при конверсии угля в метан.
Фиг.2A и 2B иллюстрируют бактериальный и архебактериальный таксономический состав репрезентативной метан-продуцирующей обогащенной культуры после 10 и 30 дней культивирования.
Фиг.3 иллюстрирует бактериальное разнообразие в конкретном образце пластовых вод по данным анализа генных последовательностей из метагенома с использованием белка RecA.
Фиг.4 иллюстрирует и приводит сравнение профиля оксигеназ в конкретных образцах пластовых вод, метан-продуцирующей обогащенной культуры и двух индивидуальных штаммах, для которых было проведено секвенирование геномов.
Фиг.5 иллюстрирует и приводит сравнение профиля оксигеназ в конкретном продуктивном пласте и образцах метан-продуцирующей обогащенной культуры.
Фиг.6 иллюстрирует и приводит сравнение профиля ответов ферментов на окислительный стресс в конкретном продуктивном пласте, метан-продуцирующей обогащенной культуре и образцах из скважины.
Фиг.7 иллюстрирует и приводит сравнение профиля ферментов метаногенеза в конкретном продуктивном пласте, метан-продуцирующей обогащенной культуре и образцах из скважины.
Фиг.8 иллюстрирует и приводит сравнение профиля эстераз в конкретном продуктивном пласте, метан-продуцирующей обогащенной культуре и образцах из скважины.
Фиг.9 иллюстрирует и приводит сравнение профиля сахаролитических ферментов в конкретном продуктивном пласте, метан-продуцирующей обогащенной культуре и образцах из скважины.
Фиг.10 иллюстрирует и приводит сравнение профиля гидрогеназ в конкретном продуктивном пласте, метан-продуцирующей обогащенной культуре и образцах из скважины.
Фиг.11 иллюстрирует и приводит сравнение профиля азотфиксирующих белков в конкретном продуктивном пласте, метан-продуцирующей обогащенной культуре и образцах из скважины.
Фиг.12 иллюстрирует и приводит сравнение профиля денитрифицирующих белков в конкретном продуктивном пласте, метан-продуцирующей обогащенной культуре и образцах из скважины.
Фиг.13 иллюстрирует увеличение продуцирования метана определенным микробным сообществом после стимуляции различными электроноакцепторами и кислородом.
Фиг.14 иллюстрирует увеличение продуцирования метана определенным микробным сообществом после стимуляции водородом и ацетатом.
Фиг.15 иллюстрирует увеличение продуцирования метана определенным микробным сообществом после стимуляции глицерином или триметиламином.
Фиг.16 иллюстрирует способ введения внешнего фактора, такого как фермент или стимулятор, в угольный пласт путем повторного закачивания пластовых вод для увеличения продуцирования метана.
Подробное описание изобретения
Настоящее изобретение предоставляет новые методы и способы стимуляции биогенного продуцирования метана в углеводородсодержащем пласте, таком как угольные пласты и скважины для добычи метана из угольных пластов, с использованием культивированных микроорганизмов, выделенных из пласта. Геномную информацию, полученную для резидентных микробных популяций, обитающих в углеводородсодержащем пласте, используют для идентификации и стимуляции ферментов, вовлеченных в различные пути метаболизма, реализуемые при конверсии углеводорода в метан, которые присутствуют в одном или нескольких микроорганизмах в пласте или вводятся в пласт, предпочтительно, вместе с идентифицированным стимулятором.
Способы согласно настоящему изобретению предоставляют постадийный подход к идентификации стимуляторов и/или определенных микробных сообществ (DMA), пригодных для увеличения биогенного продуцирования метана. Приведенные в настоящем описании примеры демонстрируют поэтапный подход в успешной идентификации стимуляторов для увеличения продуцирования метана. Коротко, в приведенных в настоящем описании примерах образцы пластовых вод отбирали из скважины для добычи метана из угольных пластов в газоносном бассейне Сан-Хуан (San Juan), где ранее проведенные исследования указали на возраст 70 миллионов лет в условиях изоляции от поверхности и отсутствия свидетельств событий подповерхностного перемешивания. Вода может быть отобрана из устья скважины, разделительного резервуара (барабанный сепаратор) или резервуара-хранилища, поскольку эти образцы воды являются наиболее легкодоступными материалами. Образцы воды, содержащие живые микроорганизмы, затем визуально исследовали с помощью световой микроскопии, и микроорганизмы культивировали с использованием пластовых вод в качестве минеральной основы. Культуры микроорганизмов обогащали (накапливали) в отношении содержания метан-продуцирующих микробов, используя уголь в качестве единственного источника углерода. В качестве стимуляторов микробного дыхания испытывали различные комбинации электроноакцепторов, таких как нитрат, сульфат или фосфат железа. Обогащенные микробные культуры затем подвергали скринингу на продуцирование метана с использованием газовой хроматографии. Состав культивированного сообщества микроорганизмов анализировали с использованием филогенетических маркеров для идентификации доминирующих групп микроорганизмов, и несколько видов микроорганизмов независимо культивировали в чистые культуры (деконволюция) для изучения их ферментных профилей, метаболизма и способности разлагать уголь. Сообщество может быть воспроизведено и составлено для оптимизированного продуцирования метана из угля (воссоздание), с образованием целенаправленно спроектированной сложной микробной экосистемы или определенного микробного сообщества (DMA).
Возможности способов согласно настоящему изобретению можно продемонстрировать путем идентификации кислорода в качестве стимулятора, увеличивающего биогенное продуцирование метана из угля. В результате идентификации присутствия большого числа оксигеназ, монооксигеназ и диоксигеназ при проведении геномных анализов образцов, кислород был идентифицирован как стимулятор. Идентификация этих ферментов была неожиданной из-за анаэробной среды, из которой были выделены микроорганизмы. Бактериальные диоксигеназы ароматических углеводородов представляют собой многокомпонентные ферментные системы, которые вводят дикислородный фрагмент в ароматическое ядро с образованием ареновых цис-диолов, в случае окисления бензола толуолдиоксигеназой до цис-1,2-дигидрокси-3,5-циклогексадиена (цис-диол из бензола) (Gibson, D.T., Cardini, G.E., Maseles, F.C., Kallio, R.E. Incorporation of oxygen-18 into benzene by Pseudomonas putida. Biochemistry. 1970. 9: 1631-1635). Другие типы оксигеназ, выявленных в геномном анализе, в обогащенной метан-продуцирующей культуре и в изолированном штамме Pseudomonas, связаны с пирокатехин-2,3-диоксигеназой. Пирокатехиндиоксигеназы представляют собой металлопротеиновые ферменты, которые осуществляют окислительное расщепление пирокатехинов. Этот класс ферментов присоединяет молекулярный кислород к субстрату. Пирокатехиндиоксигеназы принадлежат к классу оксидоредуктаз и обладают несколькими различными характеристиками субстратной специфичности, включая пирокатехин-1,2-диоксигеназу (EC 1.13.11.1), пирокатехин-2,3-диоксигеназу (EC 1.13.11.2) и протокатехат-3,4-диоксигеназу (EC 1.13.11.3). Активный центр пирокатехиндиоксигеназ наиболее часто содержит железо, но известны также марганецсодержащие формы. В реакциях, катализируемых оксигеназами, выделяется энергия, которая может быть использована для роста микроорганизмов, и в результате такого роста будут продуцироваться другие метаболиты, которые могут быть ассимилированы другими видами.
Кислород может быть релевантным газом в подземных горизонтах, поскольку было описано, что аэробные штаммы процветают в предполагаемо анаэробных средах, таких как залежи нефти (Nazina et al. The phylogenetic diversity of aerobic organotrophic bacteria from the Dagang high temperature oil field. 2007. Microbiology, 74: 343-351)). Однако в этих способах не описан механизм или принцип действия, и возможности регулировать или контролировать лежащие в их основе биологические процессы и сообщества микроорганизмов, реагирующие на такие стимулы, без такого знания ограничены.
Источники микроорганизмов и их характеристика
Как используется в данном описании, термин «углеводородсодержащий пласт» относится к любому источнику углеводородов, из которого может быть получен метан, включающему, но не ограничивающемуся ими, уголь, торф, бурый уголь, битуминозный сланец, нефтеносный пласт, традиционные тяжелые нефтяные остатки, вязкую нефть, нефтеносные пески и битуминозные пески. В обсуждаемых в данном описании различных вариантах осуществления углеводородсодержащий пласт или даже среда, окружающая углеводородсодержащий пласт, могут включать, но, не ограничиваясь ими, битуминозный сланец, уголь, угольный пласт, угольные отвалы, побочные продукты перегонки угля, бурый уголь, торф, нефтеносные пласты, битуминозные пески, загрязненную углеводородами почву, нефтяной шлам, буровой шлам и подобные, и могут также включать такие условия состояния или даже окружения в дополнение к битуминозному сланцу, углю, угольному пласту, угольным отвалам, побочным продуктам перегонки угля, бурому углю, торфу, нефтеносным пластам, битуминозным пескам, загрязненной углеводородами почве, нефтяному шламу, буровому шламу и подобным. В некоторых вариантах осуществления настоящее изобретение может предусматривать in situ (здесь: в природных условиях) углеводородсодержащий пласт, иногда называемый in situ средой, окружающей углеводородсодержащий пласт, или in situ средой продуцирования метана. Варианты осуществления могут включать ex situ (здесь: в искусственных условиях) углеводородсодержащий пласт, иногда называемый ex situ средой, окружающей углеводородсодержащий пласт, или ex situ средой продуцирования метана. Понятие “in situ” может иметь отношение к пласту или окружающей среде, в которых углеводородсодержащие источники могут находиться в их исходных местоположениях, например, in situ окружающие среды могут включать подземное месторождение. Понятие “ex situ” может относиться к пластам или условиям окружающей среды, в которых углеводородсодержащий пласт был извлечен из его исходного местоположения и необязательно может также находиться в биореакторе, ex situ реакторе, шахте, наземных конструкциях и подобных ситуациях. В качестве неограничивающего примера, биореактор может иметь отношение к любому устройству или системе, поддерживающим биологически активную среду.
При использовании угля в качестве примера углеводородсодержащего пласта, существуют многочисленные источники автохтонных микроорганизмов, которые могут играть определенную роль в конверсии углеводорода в метан, и которые могут быть проанализированы. Уголь представляет собой сложное органическое вещество, состоящее из нескольких групп мацералов, или основных типов органического вещества, которые накапливаются в различных типах условий осадконакопления, таких как торфяные болота или травяные болота. Состав мацерала и, тем самым, состав угля, изменяется в горизонтальном и вертикальном направлениях в пределах индивидуальных угольных пластов. После того, как микроорганизмы идентифицированы как содержащие фермент метаболического пути, участвующий в стадии конверсии, различные определенные микробные сообщества или стимуляторы, идентифицированные способами согласно настоящему изобретению, могут более эффективно воздействовать на конкретные группы мацералов, и поэтому каждый угольный пласт может быть уникальным в том отношении, какие типы микроорганизмов и стимуляторов являются наиболее эффективными для in situ биоконверсии угля.
Существуют многочисленные распространенные в природе микроорганизмы, ассоциированные с углем и другими осадочными породами с высоким содержанием органических веществ в подземных условиях. Со временем такие виды микроорганизмов могут стать очень эффективными в метаболизме органического вещества в подземных условиях вследствие естественного отбора. Относительно быстрая адаптация бактерий к условиям местной окружающей среды позволяет предположить, что микроорганизмы, собранные из месторождений или индивидуальных угольных пластов, могут быть генетически уникальными. После сбора проб эти микроорганизмы могут быть выращены в лабораторных культурах, как описано в данном описании, для оценки и определения факторов, увеличивающих и/или ограничивающих конверсию угля в метан. В некоторых случаях, ключевое питательное вещество или микроэлемент могут отсутствовать, и прибавление этого лимитирующего фактора может значительно увеличить продуцирование метана. Когда бактерии лишены доступа к питательным веществам, происходят физиологические изменения, и если состояние голодания продолжается, то все метаболические системы перестают функционировать, и бактерии испытывают остановку метаболизма. Когда условия окружающей среды изменяются, бактерии могут восстанавливаться и снова образовывать жизнеспособную популяцию. Таким образом, возможно, что некоторые бактерии в осадочных породах с высоким содержанием органических веществ достигли состояния остановки метаболизма, и требуется только добавление питательных веществ для активации популяции согласно настоящему изобретению. Путем специального анализа ферментов, присутствующих в таких популяциях, можно определить способы стимуляции путей метаболизма, задействованных в конверсии угля в метан, осуществляемых одним или несколькими членами этих микробных популяций.
Анаэробные бактерии из подземных горизонтов могут быть собраны несколькими разными способами, включающими: (1) добывание или отбирание образцов пластовых вод, (2) бурового шлама, (3) образцов породы со стенок скважины, (4) образцов цельного керна, и (5) образцов спрессованного цельного керна. Образцы спрессованного керна могут обеспечивать наилучшую возможность отбора жизнеспособных микробных популяций, но авторы настоящего изобретения обнаружили, что отбор микробных популяций из пластовых вод обеспечивает получение репрезентативного образца присутствующих микробных популяций. Метан-продуцирующие бактерии являются облигатными анаэробами, но могут оставаться жизнеспособными в присутствии кислорода в течение до 24 часов путем образования многоклеточных скоплений. Кроме того, бескислородные/восстановительные условия микроокружения в кислородсодержащей системе потенциально могут увеличивать срок жизнеспособности анаэробных бактерий. В некоторых случаях, буровой шлам, собранный и помещенный в анаэробные герметизированные контейнеры, будет содержать микроорганизмы, способные конвертировать уголь в метан, в течение нескольких часов, приводя, таким образом, к ошибочным результатам определения содержания газов.
Авторы настоящего изобретения оптимизировали способы отбора проб в полевых условиях для обеспечения оптимального извлечения анаэробных популяций присутствующих в них микроорганизмов. Настоящее изобретение предусматривает отбор проб микробных популяций в анаэробных условиях способами, ранее описанными в заявке PCT № PCT/US2008/057919 (WO2008/116187), и культивирование автохтонных микроорганизмов, обитающих в среде углеводородсодержащего пласта, такой как пластовые воды или скважины для добычи метана угольных пластов.
Предложенные настоящим изобретением способы также обеспечивают возможность генетических изменений микроорганизмов. Благодаря идентификации ферментативных функций в резидентных микроорганизмах и стимуляторах, которые могут быть использованы для увеличения продуцирования метана, авторы настоящего изобретения могут использовать эту информацию для генетического инжиниринга микроорганизмов для сообщения им способностей, которые могут быть связаны со стимулированием и увеличением продуцирования метана. Селекция микроорганизмов описанными в данном описании способами повышает способность эффективно метаболизировать уголь и другие субстраты с высоким содержанием органических веществ. После проведения ферментативных анализов таких обогащенных культур, можно оптимизировать целевые стимуляторы и/или генетически модифицированные бактерии. Различные возможности усиления продуцирования метана из скважин включают введение в пласт идентифицированных стимуляторов, идентифицированных микроорганизмов, определенных сообществ организмов, генетически модифицированных организмов или любых их комбинаций.
В соответствии со способами согласно настоящему изобретению, автохтонные микроорганизмы идентифицируют и затем стимулируют для превращения углеводородов в метан. Микроорганизмы, присутствующие в пласте в природных условиях, являются предпочтительными, поскольку известно, что они способны выживать и активно размножаться в условиях окружающей пласт среды, и должны обеспечивать ферментные компоненты различных путей метаболизма, начиная от гидролиза углеводородов и до метаногенеза. Однако настоящее изобретение не ограничено использованием автохтонных микроорганизмов. При анализе ферментных профилей автохтонных микроорганизмов может быть желательным объединить такую информацию с информацией, касающейся экзогенных микроорганизмов. Эта информация может быть получена из известных микроорганизмов, предпочтительно таких, которые пригодны для выращивания в подземном пласте, и которые, аналогичным образом, обладают подобным потенциалом ферментативных процессов.
Термин «определенное микробное сообщество» или «DMA», как использовано в данном описании, относится к культуре более чем одного микроорганизма, в которой различные штаммы целенаправленно комбинируют или подбирают для оптимизации преобразования углеводорода в метан. Микроорганизмы сообщества являются «определенными» в том смысле, что в любой момент времени можно определить членов популяции путем использования генетических способов, таких как таксономия по гену 16S, как описано в данном описании. DMA необязательно остаются неизменными во времени, но могут эволюционировать как постоянно изменчивые культуры для оптимизации гидролиза углеводородов и продуцирования метана. Оптимально, DMA готовят для получения микроорганизмов, обладающих профилями сильного ферментативного действия в метаболических путях преобразования углеводородов в метан. DMA могут состоять из 2 или более микроорганизмов в любых комбинациях для получения бактериальных или архебактериальных видов, способных конвертировать углеводород в любые промежуточные соединения, приводящие к образованию метана, и/или любых метаногенных видов. Например, в DMA могут присутствовать 2, 3, 4, 5, 6, 7, 8, 9, 10, 11, 12, 13, 14, 15 или более организмов. Члены DMA проявляют синергическое действие в продуцировании метана между собой или вместе с микроорганизмами, присутствующими в углеводородсодержащем пласте.
Термин «микроорганизм» предполагает включение бактерий и архебактериальных организмов, а также связанных с ними грибов, дрожжей и плесневых грибов. Следует понимать, что бактерии и архебактерии являются типичными представителями микроорганизмов вообще, которые могут разлагать углеводороды и превращать образующиеся продукты в метан. Разграничительные линии между классами микроорганизмов не всегда являются четкими, особенно между бактериями и грибами. Поэтому предпочтительно использовать термин «микроорганизмы» для включения всех микроорганизмов, которые могут преобразовывать углеводороды в метан, независимо от обычно используемых классификаций. Однако из таких микроорганизмов предпочтительными являются такие, которые обычно классифицируются как бактерии и архебактерии. Если в описываемых способах используются экзогенные бактерии и архебактерии, то также могут быть использованы другие микроорганизмы, такие как грибы, дрожжи, плесневые грибы и подобные.
Термин «анаэробный микроорганизм», как использовано в данном описании, относится к микроорганизмам, которые могут жить и расти в атмосфере, содержащей меньшее количество свободного кислорода, чем тропосферный воздух (т.е. примерно менее чем 18% моль. свободного кислорода). Анаэробные микроорганизмы включают организмы, которые могут функционировать в атмосфере с концентрацией свободного кислорода менее чем около 10% мол., или менее чем около 5% мол., или менее чем около 2% мол., или менее чем около 0,5% мол.
Термин «факультативные анаэробы», как использовано в данном описании, имеет отношение к микроорганизмам, которые могут обеспечивать протекание процессов метаболизма или расти в средах либо с высокими, либо с низкими концентрациями свободного кислорода.
Конверсия углеводородов в метан требует активного участия метан-продуцирующих бактерий. Термин «метан-продуцирующая бактерия», как использовано в данном описании, относится к облигатным и факультативным анаэробным микроорганизмам, которые продуцируют метан в результате метаболического процесса. Присутствие метан-продуцирующих бактерий в образцах указывает на высокую вероятность in situ образования метана. Метан-продуцирующие бактерии обычно классифицируют на четыре основных группы микроорганизмов: Methanobacteriales, Methanomicrobacteria и родственные, Methanopyrales и Methanococcales. Как считается, все метан-продуцирующие микроорганизмы используют для синтеза метана элементы одних и тех же биохимических превращений. Метаногенез осуществляется в результате ряда химических реакций, катализируемых металлсодержащими ферментами. Одним из путей метаболизма является восстановление CO2 до CH4 путем последовательного введения атомов водорода по одному (CO2-восстановительный метаногенез). Еще одним путем является ферментация ацетата и соединений, содержащих один атом углерода (иных, нежели метан), в метан (ферментация ацетата или ацетокластический метаногенез). Последней стадией всех известных метаболических путей метаногенеза является восстановление метильной группы до метана с использованием фермента, известного как метилредуктаза. Поскольку присутствие метилредуктазы представляет собой общую особенность всех метан-продуцирующих бактерий; оно является отличительным признаком метан-продуцирующих микроорганизмов. Предпочтительным способом идентификации присутствия метан-продуцирующих бактерий является прямое тестирование гена метан-продуцирующей бактерии, необходимого для продуцирования фермента метилредуктазы. Альтернативно, присутствие метан-продуцирующих бактерий может быть определено путем сравнения выделенной рибосомальной 16S rДНК с библиотекой архебактериальных 16S rДНК с использованием методов, известных специалисту в данной области (как правило, называемых таксономией по гену 16S).
Классы метан-продуцирующих бактерий включают, наряду с другими, Methanobacteriales, Methanomicrobacteria, Methanopyrales, Methanococcales и Methanosaeta (например, Methanosaeta thermophila). Конкретные примеры метан-продуцирующих бактерий включают Methanobacter thermoautotorophicus и Methanobacter wolfeii. Метан-продуцирующие бактерии могут также продуцировать метан путем метаболической конверсии спиртов (например, метанола), аминов (например, метиламинов), тиолов (например, метилмеркаптана), и/или сульфидов (например, диметилсульфида). Примеры таких метан-продуцирующих бактерий включают метан-продуцирующие бактерии из родов Methanosarcina (например, Methanosarcina barkeri, Methanosarcina thermophila, Methanosarcina siciliae, Methanosarcina acidovorans, Methanosarcina mazeii, Methanosarcina frisius); Methanolobus (например, Methanolobus bombavensis, Methanolobus tindarius, Methanolobus vulcani, Methanolobus taylorii, Methanolobus oregonensis); Methanohalophilus (например, Methanohalophilus mahii, Methanohalophilus euhalobius); Methanococcoides (например, Methanococcoides methylutens, Methanococcoides burtonii); и/или Methanosalsus (например, Methanosalsus zhilinaeae). Они могут также представлять собой метан-продуцирующие бактерии из рода Methanosphaera (например, Methanosphaera stadtmanae и Methanosphaera cuniculi, которые, как было продемонстрировано, метаболизируют метанол в метан). Дополнительно, они могут представлять собой метан-продуцирующие бактерии из рода Methanomethylovorans (например, Methanomethylovorans hollandica, которые, как было показано, метаболизирует метанол, диметилсульфид, метилмеркаптан, монометиламин, диметиламин и триметиламин в метан).
Как описано в данном описании, отличительным признаком настоящего изобретения является то, что микробные сообщества, полученные из разнообразных образцов окружающей среды, подлежат исследованию с использованием геномных средств, как указано выше; кроме того, микробные популяции могут быть культивированы и необязательно выделены и/или обогащены в лаборатории с использованием способов согласно изобретению. С применением таких подходов на геномном уровне и путем специфической характеристики ферментных профилей микроорганизмов, участвующих в конверсии углеводородов в метан, можно достичь фундаментального понимания метаболизма микробных сообществ и, более конкретно, метаногенного разложения угля в пластовых водах и угольных пластах. В таком случае будет возможно выяснить экологическую нишу каждой популяции и, в конечном счете, разработать стимуляторы и/или DMA, которые дадут возможность достичь увеличения биологического продуцирования метана.
В соответствии со способами согласно настоящему изобретению микроорганизмы, обитающие в среде углеводородсодержащего пласта (автохтонные микроорганизмы), и/или ферменты, присутствующие в таких микроорганизмах, идентифицируют и затем стимулируют или модулируют с целью превращения углеводородов в метан. Микроорганизмы, обитающие в природных условиях в пласте, являются предпочтительными, потому что известно, что они способны выживать и активно размножаться в среде пласта. Однако настоящее изобретение не ограничено использованием автохтонных микроорганизмов. Могут быть идентифицированы экзогенные микроорганизмы, пригодные для выращивания в подземном пласте, или могут быть идентифицированы ферменты из них, и такие микроорганизмы или ферменты вводят в пласт известными способами введения до, во время или после реализации способа согласно настоящему изобретению. Например, если пласт содержит только два микроорганизма из желательного трехкомпонентного сообщества, или только две из трех желательных ферментных функций для ферментативного пути метаболизма углеводорода в метан, то в пласт могут быть введены отсутствующие микроорганизмы, фермент или стимулятор для таких микроорганизмов или фермента. Микроорганизм, автохтонный или экзогенный, может также представлять собой рекомбинантно модифицированные или искусственные организмы.
Анализы метагенома и нуклеиновых кислот
В настоящем изобретении представлен новый подход и потенциально общий принцип увеличения продуцирования метана. Он включает описание геномов и метагеномов, наиболее фундаментальных биологических объектов в природе. Путем характеристики генома сообщества в целом, известного также как метагеном, в местах образования метана, можно достичь фундаментального понимания продуцирования метана микроорганизмами, включая используемые субстраты и образующиеся промежуточные соединения и продукты. Кроме того, могут быть выявлены взаимодействия и синергические эффекты между разными популяциями вследствие переноса электронов, которые, в конечном счете, приводят к каскадному переносу энергии в направлении к метану. Данные культивирования в комбинации с геномными результатами позволяют предположить, что микробные популяции и, вследствие этого, образование газа в подземных условиях могут быть стимулированы внешними воздействиями, состоящими во введении дополнительных субстратов, реактантов или факторов роста, и/или в засеве определенными микроорганизмами, которые приводят к увеличению продуцирования метана. Способы согласно настоящему изобретению и получаемые при их использовании результаты являются первым исследованием в области подземной микробиологии, интегрирующим метагеномику, культивирование микроорганизмов и геномный анализ выделенных штаммов. Результаты демонстрируют, что для разработки комплексного понимания экосистемы необходимо учитывать взаимозависимость этих дисциплин.
Термин «метагеном» или «метагеномика», как использовано в данном описании, относится к генетическому материалу и анализу этого генетического материала, полученному из проб окружающей среды, представляющему профиль всех микроорганизмов, присутствующих в образце. Метагеномика также называется в данной области «геномикой сообщества» или «геномикой окружающей среды». Как правило, метагеномика включает секвенирование нуклеиновой кислоты и анализ общей ДНК популяции организмов, выделенной из окружающей среды, например, коллективной ДНК, выделенной из всех микроорганизмов в образце без необходимости культивирования штаммов самих индивидуальных членов микробной популяции.
В общем, сначала выделяют ДНК из сообщества микроорганизмов в целом, т.е. метагеном, и затем амплифицируют с использованием ген-специфических праймеров (обычно, универсальных праймеров для гена 16S) и технологии полимеразной цепной реакции (ПЦР). Затем фрагменты очищают с использованием ряда методик и затем лигируют к молекулярным носителям (например, плазмидную ДНК) и трансформируют в бактерии (обычно, E. coli) как часть процесса клонирования с получением большого количества изолированных фрагментов ДНК. Культуры индивидуальных бактериальных колоний используют для выделения индивидуальных клонов (рекомбинантная плазмидная ДНК), и затем эти клоны секвенируют с использованием мишень-специфических праймеров. Полученные ДНК-последовательности затем сравнивают с ДНК-последовательностями известных штаммов по молекулярно-генетическим базам данных. В большинстве случаев, можно предположить идентичность микроорганизмов, если наблюдаются близкие совпадения с известными микроорганизмами, обладающими известными физиологическими и экологическими характеристиками.
Обычно, ДНК выделяют любыми известными в данной области способами из полученной из окружающей среды ДНК и затем разрезают на фрагменты, которые используют для составления библиотеки клона ДНК. Библиотеки клонов могут быть либо библиотеками с малыми или средними по размеру вставками (с размером вставки 2-15 т.о.), либо библиотеками с большой вставкой бактериальной искусственной хромосомы (BAC) или фосмиды (размер вставки до 150 т.о.), которые могут быть секвенированы в случайном порядке или целенаправленно.
Дальнейшие анализы метагенома включают культуро-независимый анализ 16S рРНК для определения филогенетического разнообразия (называемый 16S-таксономией), и дополнительный анализ последовательности для идентификации представляющих интерес генов в метагеноме. При секвенировании в случайном порядке клоны выбирают случайно и секвенируют с конца, и полученные последовательности собирают в большие по размеру непрерывно перекрывающиеся фрагменты («контиги») путем выравнивания перекрывающихся последовательностей. Полученные данные представляют собой контиги разной длины, а также более короткие не собранные воедино фрагменты. Наличие полностью секвенированных «эталонных» геномов может облегчить процесс сборки для близкородственных геномов. В случае их отсутствия, контиги могут быть отнесены к разным «ячейкам» на основании содержания в них G+C (гуанин+цитозин), использования кодонов, области охвата последовательности, присутствия коротких n-меров (частей нуклеотидов) и других параметров, что позволяет разделить их на группы, которые можно рассматривать в качестве «видов». Кодирующие последовательности (CDS, гены) затем прогнозируют по этим данным последовательностей различными способами. Часто в подходе случайного секвенирования идентифицированные гены не могут быть отнесены к конкретным видам микроорганизмов (т.е. таксономическая или филогенетическая привязка отсутствует), но, тем не менее, они представляют способности всего микробного сообщества и могут отображать характеристики окружающей их среды. При «целенаправленном» секвенировании клоны сначала подвергают скринингу на присутствие желательного гена (например, методом ПЦР-амплификации) или генной функции (путем функционального анализа). Секвенирование клонов-мишеней с большими вставками целиком дает возможность выделять полные опероны, например, такие, которые кодируют метаболические пути.
Общим подходом является использование в качестве мишени фосмид, несущих филогенетически информативные гены, такие как 16S рРНК. В этом способе, известном как «филогенетическая фиксация», в случае детектирования гена 16S рРНК, фосмидная вставка секвенируется целиком, что позволяет отнести геномную ДНК-последовательность к определенному филотипу. Такой подход помогает соотнести филогенез (рРНК) с предполагаемыми функциональными генами (предсказанными по фланкирующим последовательностям вставки). Фосмиды, несущие процесс-специфические или биомаркерные гены (например, для процессов, которые могут быть значительными в рассматриваемой среде, таких как окисление метана или денитрификация), могут также быть мишенями для секвенирования с целью получения дополнительной информации о путях метаболизма для этих процессов. Благодаря объединению случайного и целенаправленного подходов, представляющие интерес гены (например, гены 16S рРНК от неизвестных филотипов) или новые гены, идентифицированные на этапе случайного секвенирования, могут быть использованы для скрининга и нацеливания на другие клоны для секвенирования, или для идентификации связующих клонов и расширения охвата генома.
В одном конкретном сравнительном анализе гены, идентифицированные в метагеноме и/или представленных в нем микроорганизмах, можно сравнить с известными семействами белков для определения присутствия генных продуктов, кодирующих ферменты в метаболических путях, задействованных в конверсии углеводорода в метан. Например, база данных Pfam представляет собой большую коллекцию семейств белков, каждое из которых представлено множеством выравненных последовательностей и скрытых марковских моделей (HMM). Белки обычно состоят из одного или нескольких функциональных участков, обычно называемых доменами. Разные комбинации доменов обеспечивают многообразие белков в природе. Поэтому идентификация доменов, которые присутствуют в белках, может прояснить их функцию. См. The Pfam protein families database: R.D. Finn, J. Tate, J. Mistry, P.C. Coggill, J.S. Sammut, H.R. Hotz, G. Ceric, K. Forslund, S.R. Eddy, E.L. Sonnhammer и A. Bateman, Nucleic Acids Research, (2008), Database Issue 36: D281-D288. Путем сравнения геномной информации с базой данных Pfam, предложенные тут способы обеспечивают получение профиля ферментативных функций, присутствующих в метагеноме, индивидуальных штаммах микроорганизмов, DMA или любых их комбинациях.
Идентификация стимуляторов
Термин «стимулятор», как используется в данном описании, относится к любому фактору, который может быть использован для увеличения или стимуляции биогенного продуцирования метана в углеводородсодержащем пласте. Предпочтительно, стимулятор представляет собой субстрат, реактант или кофактор для фермента, который участвует в метаболическом пути, задействованном в конверсии углеводорода в метан. В определенных случаях стимулятор добавляют для модулирования фермента (увеличения, уменьшения или модулирования любым путем), присутствующего в обитающем в углеводородсодержащем пласте микроорганизме. В определенных случаях стимулятор может представлять собой сам фермент, микроорганизм (например, микроорганизм, экспрессирующий фермент или еще один белок, модулирующий соответствующий фермент или такой микроорганизм, полученный рекомбинантными или синтетическими методами), или определенное микробное сообщество. В любом случае, назначение стимулятора заключается в усилении имеющегося продуцирования путем повышения уровня активности или роста микроорганизма, или в увеличении, снижении или любом модулировании ферментативной активности фермента, участвующего в пути метаболизма, задействованном в конверсии углеводорода в метан, чтобы оптимизировать конечное продуцирование метана из углеводородсодержащего пласта.
Стимуляторы могут обеспечивать усиление действия, замену, или добавление любого фермента, не являющегося оптимально представленным или функциональным в углеводородсодержащей среде. Цель заключается в оптимизации и/или завершении пути метаболизма углеводорода в метан. В общем, это требует предоставления ферментов или микроорганизмов, экспрессирующих ферменты, которые способны конвертировать углеводород в продукт, такой как водород, диоксид углерода, ацетат, формиат, метанол, метиламин или любой другой метаногенный субстрат, и метаногенных ферментов. Общие категории ферментов включают ферменты, способные осуществлять гидролиз низкосортного угля, деполимеризацию угля, анаэробное или аэробное разложение полиароматических углеводородов, гомоацетогенез и метаногенез (включая гидрогенотрофный или CO2-восстановительный и ацетокластический), и любые их комбинации для достижения конверсии углеводорода в метан. Ферменты, обеспечивающие такие функции, могут включать, например, пероксидазы, фенолоксидазы, алкогольоксидазы, лакказы, гидролазы, гликозилгидролазы, эстеразы, этеразы, оксидазы, нитрогеназы, целлюлазы, амилазы, глюканазы, пулланазы, редуктазы, дисмутазы, оксигеназы, монооксигеназы, диоксигеназы, каталазы, гидрогеназы и карбоксилазы.
Примеры стимуляторов включают лиофилизированные микроорганизмы, такие как метан-продуцирующие бактерии, синтрофы, ферментативный и/или гидролитический микроорганизм; или стимулятор, субстрат, реактант или кофактор может иметь химическую природу, включая такие соединения, как азот, фосфор, калий, витамины, металлические микроэлементы, дрожжевой экстракт, серосодержащее соединение, азотсодержащее соединение, фосфорсодержащее соединение, микроэлемент, электроноакцептор, электронодонор, галоген, металл, спирт, органическая кислота, алкан, алкен, алкин, ароматическое соединение, амин, простой эфир, альдегид, кетон, тиол, ацетат, ароматический углеводород и газ.
После идентификации фермента способом согласно настоящему изобретению могут быть идентифицированы соответствующие субстрат, реактант или кофактор для этого фермента.
Конкретные стимуляторы включают, например, дрожжевой экстракт, NH4Cl, NaNO3, K2HPO4, кофермент M, PO4, витаминную смесь без фосфата, металлические микроэлементы, O2, H2, фосфористые соединения, молочную кислоту, минеральные почвенные структурообразователи (такие как хлоридные, аммониевые, фосфатные, натриевые, калиевые, магниевые и кальциевые), металлсодержащие добавки (такие как Mn, Fe, Co, Zn, Cu, Ni, Se, W или Mo), витаминные добавки (такие как пиридоксим, тиамин, рибофлавин, кальций, пантотенат, липоевая кислота, парааминобензойная кислота, никотиновая кислота, витамин B12, биотин, фолиевая кислота и меркаптогептансульфоновая кислота, пируват, алифатические спирты, метанол, этанол, 2-пропанол, 2,3-бутандиол, ваниллат, глицин, цистеин, формиат, этаноламин и 3,4,5-триметоксибензоат, водосодержащие добавки, формиат, ацетат, лактат, пируват, NaCl, целлюлоза, раствор минеральных веществ, коричная кислота, бензойная кислота, 1,2-динитроглицерин (DNG), аласан (биоэмульгатор), композиция удобрения, хитин, хитозан, хлорат, перхлорат и любые их комбинации.
Введение стимуляторов для увеличения продуцирования метана
Способы и методы согласно настоящему изобретению могут быть легко использованы в полевых условиях и для увеличения in situ или ex situ образования метана из любого углеводородсодержащего пласта, такого как уголь. Существует несколько способов или комбинация методов введения, известных в данной области, которые могут быть использованы in situ. Стимуляторы, DMA или микроорганизмы, идентифицированные способами согласно настоящему изобретению, могут быть введены непосредственно в трещины в пласте. Должны учитываться такие факторы, как ориентация разломов, in situ направление распространения напряжений в настоящий момент, геометрия продуктивного пласта (угля и/или сланца) и локальное строение. Например, в угольных пластах существует две основные сети трещин (называемые зонами кливажа), называемые системами главного кливажа и второстепенного кливажа. Зоны главного кливажа часто являются более протяженными в горизонтальном направлении и проницаемыми, в то время как зоны второстепенного кливажа (которые примыкают к зонам главного кливажа), являются менее протяженными и проницаемыми. При стимуляции скважин для добычи метана угольных пластов искусственно создаваемые трещины пересекаются с первичными зонами главного кливажа, обеспечивая улучшенный доступ к продуктивному пласту. Однако в тех случаях, когда существующее в данный момент in situ направление распространения напряжений перпендикулярно зонам главного кливажа, давление напряжения сдавливает зоны главного кливажа, тем самым уменьшая проницаемость, но, в то же время, in situ давление увеличивает проницаемость системы второстепенного кливажа. В таких условиях, искусственно созданные трещины перпендикулярны к направлению второстепенного кливажа, обеспечивая лучший доступ к природной системе трещин продуктивного пласта. Геометрия нагнетающей и продуктивной скважин и использование или неиспользование горизонтальных шурфов для доступа к продуктивному пласту, зависят преимущественно от местных геологических и гидрологических условий.
Целью стимуляции выхода метана угольных пластов методом гидроразрыва, как в обычных нефтяных и газовых скважинах, является создание искусственной сети трещин, которая соединяется с природной сетью трещин продуктивного пласта. Стимуляторы, DMA или микроорганизмы, идентифицированные способами согласно настоящему изобретению, могут быть введены в природные и искусственно сформированные трещины под давлением для нагнетания смеси в природные трещины вглубь продуктивного пласта для увеличения скоростей биоконверсии и эффективности. При стимуляции продуктивных пластов путем гидроразрыва песчаный агент для расклинивания трещин и различные химические вещества могут быть закачаны в пласт под высоким давлением через буровую установку.
Стимуляторы, DMA или микроорганизмы могут быть введены под давлением в продуктивный пласт одновременно со стимулированием методом гидроразрыва и/или после образования трещин гидроразрыва. Как предполагается, основная часть in situ деятельности микроорганизмов будет происходить после стимуляции методом гидроразрыва и удаления текучих сред для закачивания скважины, когда будут восстановлены анаэробные условия подземной среды. Однако при одновременном in situ микробной стимуляции и возбуждении гидроразрывом, предпочтительным является использование текучих сред для стимуляции в бескислородных или малокислородных условиях, чтобы поддерживать анаэробные условия в продуктивном пласте, или оно может быть без труда реализовано после стимуляции. Нагнетание аэробных бактерий при одновременной стимуляции будет приводить к быстрому расходованию кислорода и возврату к анаэробным условиям.
В некоторых случаях, вместе с текучими средами для гидроразрыва пласта могут быть использованы текучие среды для предварительной обработки, которые модифицируют уголь, углистый сланец или сланец с высоким содержанием органических веществ для биоконверсии. Однако предпочтительным способом стимуляции in situ биоконверсии органического вещества является нагнетание стимуляторов, DMA или микроорганизмов под давлением и в анаэробных условиях после стимуляции гидроразрывом и последующей промывки скважины.
Стимуляторы, DMA или микроорганизмы, идентифицированные способами согласно настоящему изобретению, могут быть введены путем повторного закачивания пластовых вод под землю, как изображено на фиг.16. Коротко, метан и пластовые воды выкачивают из обсадной трубы 1 скважины в разделительный резервуар 2 (известный также как барабанный газоотделитель) для удаления газа из воды. Пластовые воды хранят в резервуаре-хранилище 3, из которого они могут быть направлены в накопительную станцию или поданы для повторной закачки под землю. Затем стимуляторы, DMA или микроорганизмы могут быть добавлены в подготовительный резервуар 4 и смешаны с извлеченными пластовыми водами. Затем компрессор 5 или напорная система могут быть использованы для закачки стимуляторов, DMA или микроорганизмов в пластовых водах под землю.
Растворенный in situ кислород, присутствующий в пластовых водах, может не быть доступным для микроорганизмов в угольных пластах и, тем самым, становится ограничивающим фактором для повышения продуцирования метана. Введение стимуляторов, DMA или микроорганизмов, или подача газов, жидкостей, гелей или твердых веществ могут создавать среду, пригодную для увеличения продуцирования метана, включая штаммы, способные к аэробному разложению углеводородов, связанных с кислородом. Например, в примере варианта осуществления посевной материал, состоящий из подходящих автохтонных штаммов, таких как Pseudomonas, в количестве 107 клеток на мл, может быть смешан с гелем, состоящим из органических субстратов, таких как глицерин, которые могут быть использованы в качестве питательных веществ, стимулирующих рост путем ферментации и секреции метаболитов, включая водород, который может быть использован метан-продуцирующими бактериями. После ассимиляции геля, он будет медленно выделять оптимальные количества кислорода, который, в свою очередь, будет использоваться штаммами, способными к аэробному разложению углеводородов. Такие добавки и создаваемый в результате метаболизм будут стимулировать перенос электронов, способствующий увеличению продуцирования метана и выхода, по сравнению с контрольными скважинами в этом же пласте, которые не подвергались воздействию. Это особенно предпочтительно для штаммов, обладающих способностью к росту в аэробных или анаэробных условиях, и которые могут адаптировать свой метаболизм для разложения углеводородов. В отдельном варианте осуществления пластовые воды с высокой концентрацией растворенного кислорода нагнетают в скважину с целью подачи некоторого количества кислорода, необходимого для катализируемых оксигеназой реакций. Кислород может быть растворен в пластовых водах путем аэрации с помощью механических систем, таких как турбинные мешалки или другие механизмы. Альтернативно, для подачи кислорода в анаэробную среду может быть использован промежуточный механизм. Например, для стимуляции выделения кислорода ферментами хлоратредуктазой и хлоритдисмутазой, присутствие которых было определено при проведении анализов метагенома, в качестве электроноакцептора может быть использован хлорат.
В альтернативном варианте осуществления способ, основанный на использовании частиц, может быть применен для распределения стимуляторов, DMA или микроорганизмов (в совокупности, средства воздействия) во время проведения гидроразрыва. Цель заключается в использовании таких средств воздействия для обеспечения устойчивого увеличения продуцирования метана. Усовершенствованная система подачи нагнетает средства глубоко в трещины скважины и обеспечивает распределение с замедленным во времени высвобождением. Например, средство воздействия для скважины может быть приготовлено либо в виде покрытия с пролонгированным высвобождением на зернах песка, используемого в процессе гидроразрыва, либо в виде твердых частиц, которые медленно растворяются со временем; предусматривается, что они будут иметь приблизительно такой же размер, как зерна песка, используемого в процессе гидроразрыва, и могут быть смешаны вместе перед добавлением в раствор гуаровой смолы, известный как проппант. В любом варианте осуществления, после нагнетания проппанта и частиц в скважину под давлением, зерна песка с покрытием или твердые частицы, смешанные с песком, нагнетают под давлением в трещины скважины, поддерживая их в открытом состоянии для облегчения выхода газа или нефти. Поскольку средства воздействия приготовлены в расчете на долговременное высвобождение, подобно некоторым фармацевтическим препаратам, соединения и/или микробы будут медленно растворяться и диффундировать в окружающие пластовые воды и зоны кливажа в угле (или в тонкие трещины скальной породы в случае нефти), где предположительно обитают прикрепленные бактерии. Таким образом, растворяющиеся средства непрерывно стимулируют биогенную конверсию угля в метан. Композиции могут быть составлены таким образом, чтобы обеспечить высвобождение средства воздействия на протяжении периода времени в несколько часов, дней, недель или месяцев, с целью оптимизации процесса стимуляции выделения метана. Покрытия или частицы могут быть приготовлены в условиях отсутствия кислорода для поддержания жизнеспособности строго анаэробных микроорганизмов, или они могут также содержать газы, которые стимулируют продуцирование метана.
Приведенные ниже примеры предназначены для иллюстрации изобретения, но не его ограничения.
Пример 1
Отбор проб и накопление метан-продуцирующих микроорганизмов из скважин для добычи метана угольных пластов
Пластовые воды в объеме 200 л отбирали из резервуара-хранилища и в объеме 20 л из отстойника на скважине для добычи метана угольных пластов, расположенной в месторождении Сан-Хуан, Колорадо, США. Затем образцы воды фильтровали через серию стерильных сит с размерами отверстий от 1 мм до 45 мкм для удаления крупных частиц угля и нефтепродуктов, поступающих вместе с пластовыми водами. Затем часть образца переносили в стерильную бутылку емкостью 1 л, и через ее содержимое барботировали азот (N2) с использованием переносного резервуара и стеклянной пипетки. Затем бутылки герметично закупоривали пробками из бутилкаучука и использовали для инокуляции.
Среда состояла из минеральной основы и сырого угля в качестве источника углерода, дозированных в пробирки Хангейта с 5 мл культуры и 0,5 г угля в качестве единственного источника углерода.
Состав среды для накопления метан-продуцирующих бактерий и чистых культур:
На 1 л стерильной пластовой воды:
| NH4Cl | 0,5 г |
| KH2PO4 | 0,75 г |
| K2HPO4 | 1,5 г |
коммерческий (из коллекции ATCC) раствор витамина и микроэлемента по 10 мл каждого.
Стерилизовали при давлении 1 атм (101,32 кПа) в течение 15-30 минут и затем добавляли из маточного раствора:
дрожжевой экстракт до конечной концентрации 0,05%
Na2S×9H2O до конечной концентрации 3 мМ
цистеин-HCl до конечной концентрации 3 мМ.
Стерилизовали при давлении 1 атм (101,32 кПа) в течение 15-30 минут и затем добавляли из маточного раствора:
надлежащий источник углерода и энергии для метаногенеза:
газовая смесь CO2:H2/20:80 до давления 2 атм (202,64 кПа).
В некоторых культурах для стимуляции анаэробного дыхания и роста была использована смесь электроноакцепторов, состоящая из нитрата натрия (10 мМ), сульфата натрия (10 мМ) и фосфата железа (10 мМ). Среду готовили анаэробно путем дозирования всех компонентов в анаэробной камере с атмосферой из 5% H2, 5% CO2, и остальное N2. Другие культуры включали использование автоклавированного угля. Для приготовления сред не использовали восстановительные реагенты, такие как сульфид натрия или цистеин. Образцы инокулировали непосредственно в полевых условиях путем отбора в анаэробных условиях 1 мл из бутылок для образцов емкостью 1 л с помощью шприца и иглы, которые предварительно трижды продували азотом. Инокулированные пробирки инкубировали при температуре 30°C и направляли в лабораторию. После нескольких недель выращивания образцы обследовали на наличие роста с использованием микроскопа, и продуцирование метана измеряли с помощью газовой хроматографии. Улучшенные образцы отбирали по их способности расти на угле в качестве единственного источника углерода и по уровню продуцирования ими метана. Наивысшая концентрация метана была определена у культур, где электроноакцепторы отсутствовали. После шести последовательных пересевов первичного обогащенного образца, продуцирование метана становилось, по наблюдениям, воспроизводимым и масштабируемым, устойчиво давая содержание 3% в паровоздушном пространстве. Сообщество, выбранное для продолжения характеризации, переносили затем во флаконы для сыворотки, и продуцирование метана происходило стабильно на уровне около 3% в паровоздушном пространстве в течение от 10 до 30 дней при температуре 30°C.
Пример 2
Характеристика сообщества микроорганизмов из скважины для добычи метана угольных пластов и накопление метан-продуцирующих микроорганизмов
Общую ДНК сообщества экстрагировали из образцов пластовых вод способами, оптимизированными для эффективного отделения нуклеиновых кислот от угля, присутствующего в пластовых водах и обогащенных образцах. Геномные библиотеки были составлены из образца воды из резервуара-хранилища с использованием различных способов для оценки потенциальных систематических ошибок и для эффективного охвата всех популяций микроорганизмов, включая бактерии, архебактерии и эукариоты. Предшествующие геномные анализы на образцах из резервуара-хранилища выявили относительно низкую степень сложности по сравнению с такими окружающими средами, как почвы или вода морской поверхности. Примечательной особенностью было отсутствие эукариотических клеток. В геномных данных наблюдались две доминирующих клеточных линии, соответствующих Proteobacteria, Arcobacter и Chrysiogenes, геномы которых могут быть повторно собраны из ДНК сообщества. Их метаболизм может быть ассоциирован с разложением нефтепродуктов и других углеводородов и с дыханием в присутствии арсенитов.
Получение ДНК
Воду, пропущенную через сито с размером отверстий менее 45 мкм, затем фильтровали с помощью серии соединенных последовательно мембран с размерами пор 3, 0,8 и 0,1 мкм. Мембраны извлекали из фильтровального аппарата, замораживали с буфером Tris-EDTA при температуре -20°C и направляли в лабораторию. ДНК экстрагировали из мембран следующим образом.
Фильтры промывали в течение 45 минут при комнатной температуре на вращающемся колесе в избыточном объеме лизисного буфера (50 мМ NaCl, 50 мМ Tris с pH 8,0, 50 мМ EDTA, 5% SDS, 4% поливинилпирролидона, 1% полиэтиленгликоля (8000), 0,5 M глюкозы, 200 мМ бета-меркаптоэтанола, 10 мМ спермидина, 10 мМ аскорбиновой кислоты, 20 мкг/мл бис-бензамида и 100 мкг/мл дрожжевой тРНК). С каждого образца собирали супернатанты, и клетки разрушали добавлением к каждому образцу пяти шариков из нержавеющей стали диаметром 1/8 дюйма (3,175 мм) и одного с диаметром 3/8 дюйма (9,525 мм), а также 1 г стеклянных бусин размером 0,5 мм, и встряхиванием образцов в течение 4 минут при 1500 тактов в минуту в аппарате Geno/Grinder 2000. К каждому образцу добавляли хлорид натрия до концентрации 0,8M, образец однократно экстрагировали смесью «фенол-хлороформ», один раз хлороформом, и осаждали их изопропанола.
В качестве альтернативы фильтрации, сначала из пластовых вод выделяли осадок путем центрифугирования при скорости 10000 об/мин в течение 30 минут при температуре 4°C, супернатант удаляли в свежий контейнер, осадок клеток/обломков суспендировали в лизисном буфере, и ДНК очищали таким же образом, как описано выше. Остаточный биологический материал извлекали из надосадочной жидкости добавлением полиэтиленгликоля 8000 до концентрации 10%, инкубированием при температуре 4°C в течение ночи и затем центрифугированием при скорости 10000 об/мин в течение 30 минут при температуре 4°C, суспендированием осадка в лизисном буфере и повторением описанной выше методики очистки. Полученную в результате очищенную ДНК растворяли в малом объеме 10 мМ Tris с pH 8,0, 1 мМ EDTA, и анализировали методами спектроскопии и гель-электрофореза.
Составление геномной библиотеки
Геномную библиотеку составляли путем разрезания метагеномной ДНК из пула описанных выше микроорганизмов на фрагменты со средним размером 1-8 т.о. с помощью устройства GeneMachines HydroShear для геномных растворов, оборудованного стандартным блоком для создания сдвиговых нагрузок. ДНК сортировали по размеру на агарозных гелях, присоединяли к держателям для ДНК и лигировали в клонирующий вектор E.coli со средним числом копий с использованием стандартных процедур, известных в данной области. Продукт лигирования трансформировали в E. coli методом электропорации, отбирали случайные клоны, выращивали в 1 мл культурах и экстрагировали плазмидную ДНК. Каждый клон секвенировали двунаправленно по методу Сангера.
Анализы последовательности
Таксономическое разнообразие пластовых вод (резервуар-хранилище) анализировали сравнением 16S генных последовательностей либо непосредственно из метагенома (последовательности из библиотеки окружающей среды), либо путем амплификации 16S генной последовательности из образцов ДНК, использованных для составления библиотеки метагенома. Эти анализы показали, что сообщество состояло из архебактерий и бактерий, но эукариотические клетки не присутствовали.
Результаты анализов индивидуальных метагеномов затем подвергали конвейерной обработке с помощью специализированной системы биоинформационного аннотирования, которая сначала идентифицировала все открытые рамки считывания (ORF) размером более 50 аминокислот. Для отнесения предполагаемых функций к каждой ORF, их сначала анализировали на принадлежность к семействам PFAM, TIGRFAM и SUPERFAM по имеющимся на данный момент коллекциям множественных выравниваний последовательностей и скрытых марковских моделей для соответствующих семейств белков с помощью прикладной программы HMMER. Дополнительно, программу BLASTp использовали для сравнения белков, идентифицированных в метагеноме, с безизбыточной базой данных белков при базе данных GenBank. Затем проводили поиск по аннотациям, полученным при такой конвейерной обработке, и сравнение метагенома из резервуара-хранилища, метан-продуцирующих обогащенных культур и выделенных штаммов. Анализы выявили большое число генов, которые нуждаются в кислороде, таких как диоксигеназы (нитропропан, фитаноил-CoA, толуат, бифенил-2,3-диол и дитерпеноид) и монооксигеназы (P450, алкан-, аммиак- и 2,4-дихлор-). Наряду с ферментами, нуждающимися в кислороде, было найдено также значительное число ферментов, обеспечивающих защиту от кислорода, таких как каталазы, супероксиддисмутаза, рубредоксин и тиоредоксин.
Метан-продуцирующие обогащенные культуры анализировали таксономически с использованием 16S генных последовательностей для доменов Bacteria (бактерии) и Archaea (архебактерии), последний из которых содержит метан-продуцирующие бактерии. Сообщество анализировали после 10 и 30 дней инкубации путем амплификации этого фрагмента сообщества, создания библиотеки 16S фрагментов путем клонирования их в вектор, его трансформации в E. coli и секвенирования клонированных фрагментов, как описано выше. Эти последовательности затем сравнивали с опубликованными базами данных для определения ближайших культивируемых родственных культур. Как показано на фиг.2A, в бактериальном разнообразии доминировали организмы, относящиеся к Pseudomonas, Desulfuromonas, Pelobacter, Desulfovibrio, после 10 дней, и Spirochaeta, Erysipelothrix, Thauera, Clostridium, Acholeplasma и Magnetospirillum были менее распространенными через 10 или 30 дней. Как показано на фиг.2B, в архебактериальной популяции доминировала метан-продуцирующая бактерия Methanolobus на день 10, и на 30-й день Methanocalculus, и появлялся неохарактеризованный Crenarcheaota. Фиг.3 иллюстрирует бактериальное разнообразие в конкретном образце пластовых вод при проведении анализа по генным последовательностям RecA из метагенома.
Образцы из устья скважины - представители бактериальной 16S таксономии
Dictyoglomus
Planctomycetaceae
Rubrobacteraceae
Thermodesulfovibrio
Clostridiales
Bacteroidales
Thermacetogenium
Thermotoga
Thermosediminibacter
Deltaproteobacteria
Syntrophomonas
Bacteroidetes
Bacteroidales
Termodesulfovibrio
Magnetobacterium
Sporomusa
Deferribacteraceae
Thermotoga
Clostridiales
Sulfurospirillum
Proteiniphilum
Coprothermobacter
Anaerosinus
Azospira
Ceillonellaceae
Nitrospiracaea
Thermoanaerobacterium
Ruminococcaceae
Clostridia
Therminocola
Peptococcaceae
Clostridiales
Proteobacteria
Ralstonia
Ruminococcaceae
Bactersidales
Propionibacteriaceae
Niastella
Serratia
Thermodesulfovibrio
Niastella
Chryseobacterium
Smithella
Gammaproteobacteria
Magnetobacterium
Proteiniphilum
Spirochaetaceae
Представители архебактериальной 16S таксономии - метаногенез
Thermoprotei
Methanothrix
Methanofollis
Methanobacterium
Methanomicrobiales
Methanocorpusculum
Desulfurococcales
Выделение штамма
Функциональное обогащение и пробы окружающей среды были использованы для выделения индивидуальных штаммов путем компартментализированного культивирования микроорганизмов окружающей среды (EMCC, как описано в PCT/US2008/057919, WO2008/116187), или стандартными способами, такими как встряхивание на агаре. Способ EMCC осуществляли путем инкапсулирования суспензии клеток в гелевых микрокапельках (GMD) и инкубации в аэробных условиях при температуре 30°C. Клетки образовывали колонии, которые сортировали на стерильной среде для субкультивирования. Полученные клеточные культуры затем анализировали по 16S для идентификации уникальных штаммов. Последний способ заключался в использовании плавленого агара, на который наносили суспензию клеток из серии разведений. Пробирки затем закупоривали, и газовую среду над образцом заменяли N2:CO2 или H2:O2, и инкубировали до начала образования колоний клеток, которые отбирали и субкультивировали. Выбранные выделенные штаммы затем культивировали в анаэробных условиях, причем некоторые из них были способны расти либо в аэробных, либо в анаэробных условиях.
Для выделения индивидуальных штаммов из метан-продуцирующей обогащенной культуры, 100 мкл образца разводили и инокулировали в пробирки Хангейта с агаром и углем для образования колоний и обеспечения возможности выделения конкретных линий. Дополнительно, обогащенную культуру инкапсулировали и инкубировали в аэробных условиях для образования микроколоний, которые высеивали на 96-луночные планшеты высокоскоростного устройства для сортировки клеток. Такие методики выделения привели к получению штаммов, которые затем были идентифицированы с помощью 16S генных последовательностей (как показано в фиг.2A и 2B). Из этой исходной метан-продуцирующей обогащенной культуры выращивали индивидуальные штаммы Pseudomonas, Desulfuromonas, Pelobacter, Desulfovibrio, Thauera, Acholeplasma и Methanocalculus pumilus. Индивидуальные штаммы затем могут быть восстановлены в сообщества в функционально обогащенной культуре, как определенные микробные сообщества. Некоторые выделенные штаммы также использовали для секвенирования генома с целью идентификации генов и путей метаболизма, задействованных в разложении угля. Например, штамм Pseudomonas содержал оксигеназы, принимающие участие в разложении некоторых полициклических ароматических углеводородов (PAH), такие как 3-фенилпропаноатдиоксигеназа, алкансульфонатмонооксигеназа и пирокатехин-2,3-диоксигеназа, наряду с другими.
Выделенные клеточные культуры - 16S таксономия
| Отнесены к родам (16S) | Клеточные культуры | Отнесены к родам (16S) | Клеточные культуры |
| Acetobacterium | 5 | Nitrospira | 1 |
| Acholeplasma | 1 | Paenibacillus | 3 |
| Achromobacter | 5 | Paludibacter | 1 |
| Acinetobacter | 1 | Pannonibacter | 2 |
| Aeromonas | 97 | Parabacteroides | 3 |
| Aquimonas | 1 | Petrotoga | 1 |
| Azoarcus | 2 | Pseudomonas | 1636 |
| Azonexus | 1 | Raoultella | 3 |
| Azospira | 82 | Rhodobacter | 2 |
| Bacillus | 47 | Rhodopseudomonas | 1 |
| Brevibacillus | 15 | Shewanella | 44 |
| Burkholderia | 1 | Staphylococcus | 1 |
| Butyrivibrio | 2 | Sulfurospirillum | 23 |
| Carnimonas | 2 | Thalassospira | 7 |
| Citrobacter | 9 | Thauera | 2 |
| Delftia | 2 | Thiobacillus | 1 |
| Desulfovibrio | 2 | Tistrella | 2 |
| Devosia | 2 | неклассифицированные «Bacillaceae 2» | 1 |
| Dysgonomonas | 3 | неклассифицированные Bacillus | 33 |
| Enterobacter | 5 | неклассифицированные Bacteroidales | 2 |
| Ewingella | 12 | неклассифицированные Enterobacteriaceae | 1 |
| Geobacillus | 43 | неклассифицированные Rhodocyclaceae | 1 |
| Halomonas | 3 | неклассифицированные Rikenellaceae | 3 |
| Halovibrio | 1 | неклассифицированные Sphingomonadaceae | 1 |
| Hyphomonas | 1 | неклассифицированные Xanthomonadaceae | 1 |
| Levilinea | 1 | Vibrio | 2 |
| Methanocalculus | 1 | Wolinella | 2 |
| Micrococcineae | 1 |
Культивирование толерантных к кислороду штаммов микроорганизмов из пластовых вод
Инокуляция анаэробно отобранных пластовых вод в аэробные среды приводила к росту различных клеточных линий, способных ассимилировать экзогенные источники углерода, такие как дрожжевой экстракт, но при этом способных расти на пластовых водах и сыром угле в качестве единственного источника углерода. Это позволяет предположить, что в среде существуют клетки с генетическим и физиологическим потенциалом аэробного разложения углеводородов. Такие штаммы включают генетически неоднородные члены группы Pseudomonas, такие как Pseudomonas sp., Pseudomonas 3CB6, Pseudomonas sp. SCT, Pseudomonas sp. G-R2A7 и другие, такие как Hvphomonas polymorpha, Staphylococcus haemolyticus, некультивируемая бактерия, некультивируемая денитрифицирующая бактерия (Thalassospira, Pannonibacter phragmatis (Achromobacter), Azoarcus (Betaproteobacteria), Tistrella mohilis, и некультивируемая бактерия (Thaurea). Многие из них могут расти в присутствии угля в качестве единственного источника углерода и продуцировать значительные количества биомассы.
Участки локализации метана угольных пластов и связанные с ними пластовые воды считаются бескислородными, и современные парадигмы указывают, что доминирующий метаболизм, по-видимому, связан с ферментацией и анаэробным дыханием нитратных, сульфатных и других концевых электроноакцепторов, но не с кислородом. Однако метагеномные анализы пластовых вод показали, что микроорганизмы могут быть пригодны для культивирования с использованием пластовых вод в качестве минеральной основы и угля в качестве единственного источника углерода, и различных комбинаций электроноакцепторов, включая кислород, нитрат, сульфат или фосфат железа, для стимуляции дыхания микроорганизмов. Как показано на фиг.4, широкий спектр монооксигеназ и диоксигеназ был обнаружен в образцах пластовых вод, обогащенных метан-продуцирующих культур, а также в выделенных штаммах Pseudomonas и Thallasospira.
Идентификация ферментных семейств
Метагеномные данные, полученные для образцов продуктивного пласта и обогащенных метан-продуцирующих культур, позволили идентифицировать несколько классов ферментов, которые могут быть использованы для воздействия с целью увеличения продуцирования метана в углеводородсодержащих пластах. В приведенной ниже таблице 1 представлены данные Pfams для идентифицированных ферментных семейств, которые функционируют на различных ферментативных стадиях конверсии углеводорода в уголь. Фиг.5-12 дополнительно иллюстрируют разнообразие ферментов, идентифицированных в ряде Pfams.
| ТАБЛИЦА 1 | ||
| Метаболический процесс | Организм | Фермент |
| Гидролиз низко-сортного угля | Dictyoglomus Thermotoga Desulfurococcales |
PF02446 4-альфа-глюканотрансфераза PF05448 Ацетилксиланэстераза (AXE1) PF02806 Альфа-амилаза, C-концевой алло-бета домен PF02903 Альфа-амилаза, N-концевой ig-подобный домен PF09261 Альфа-маннозидаза, средний домен PF07821 Альфа-амилаза C-концевой бета-листовой домен PF09071 Альфа-амилаза, C-концевой PF05270 Альфа-L-арабинофуранозидаза B (ABFB) PF09206 Альфа-L-арабинофуранозидаза B, каталитическая PF06964 Альфа-L-арабинофуранозидаза C-конец PF08531 Альфа-L-рамнозидаза N-концевой домен PF06202 Амило-альфа-1,6-глюкозидаза PF05592 Бактериальная альфа-L-рамнозидаза PF05592 Бактериальная альфа-L-рамнозидаза PF03714 Бактериальная пулланаза-ассоциированный домен PF02929 Бета-галактозидаза, малая цепь PF02449 Бета-галактозидаза PF08533 Бета-галактозидаза, C-концевой домен PF08532 Бета-галактозидаза, домен тримеризации PF03856 Бета-глюкозидаза (семейство SUN) |
| PF02018 Углевод-связывающий домен PF02839 Углевод-связывающий домен PF03425 Углевод-связывающий домен (семейство 11) PF03426 Углевод-связывающий домен (семейство 15) PF03424 Углевод-связывающий домен (семейство 17/28) PF03427 Углевод-связывающий домен (семейство 19) PF03423 Углевод-связывающий домен (семейство 25) PF09478 Углевод-связывающий домен CBM49 PF03422 Углевод-связывающий модуль (семейство 6) PF09212 Углевод-связывающий модуль 27 PF00553 Целлюлозу-связывающий домен PF00942 Целлюлозу-связывающий домен PF02013 Целлюлозу- или белок-связывающий домен PF01607 Хитин-связывающий перитрофин-A домен PF00182 Хитиназа, класс I PF03174 Хитобиаза/бета-гексозаминидаза C-концевой домен PF06452 Домен неизвестной функции (DUF1083) PF09081 Домен неизвестной функции (DUF1921) PF09154 Домен неизвестной функции (DUF1939) PF09260 Домен неизвестной функции (DUF1966) PF02056 Семейство 4 гликозилгидролазы PF00734 Грибковый целлюлозу-связывающий домен |
| PF09137 Глюкодекстраназа, домен N PF07915 Глюкозидаза II, бета-субъединице-подобный белок PF03198 Гликолипид-фиксированный поверхностный белок PF00232 Гликозилгидролаза семейство 1 PF00331 Гликозилгидролаза семейство 10 PF01670 Гликозилгидролаза семейство 12 PF01373 Гликозилгидролаза семейство 14 PF00728 Гликозилгидролаза семейство 20, каталитический домен PF02838 Гликозилгидролаза семейство 20, домен 2 PF02156 Гликозилгидролаза семейство 26 PF01915 Гликозилгидролаза семейство 3 C-концевой домен PF00933 Гликозилгидролаза семейство 3 N-концевой домен PF02015 Гликозилгидролаза семейство 45 PF01374 Гликозилгидролаза семейство 46 PF01532 Гликозилгидролаза семейство 47 PF02011 Гликозилгидролаза семейство 48 PF03718 Гликозилгидролаза семейство 49 PF03512 Гликозилгидролаза семейство 52 PF07745 Гликозилгидролаза семейство 53 PF03065 Гликозилгидролаза семейство 57 PF02057 Гликозилгидролаза семейство 59 PF03443 Гликозилгидролаза семейство 61 |
| PF03664 Гликозилгидролаза семейство 62 PF03632 Гликозилгидролаза семейство 65 центральный каталитический домен PF03633 Гликозилгидролаза семейство 65, C-концевой домен PF03636 Гликозилгидролаза семейство 65, N-концевой домен PF07477 Гликозилгидролаза семейство 67 C-конец PF07488 Гликозилгидролаза семейство 67 средний домен PF03648 Гликозилгидролаза семейство 67 N-конец PF00840 Гликозилгидролаза семейство 7 PF02324 Гликозилгидролаза семейство 70 PF03659 Гликозилгидролаза семейство 71 PF03663 Гликозилгидролаза семейство 76 PF03662 Гликозилгидролаза семейство 79, N-концевой домен PF03639 Гликозилгидролаза семейство 81 PF03644 Гликозилгидролаза семейство 85 PF07470 Гликозилгидролаза семейство 88 PF00759 Гликозилгидролаза семейство 9 PF07971 Гликозилгидролаза семейство 92 PF08306 Гликозилгидролаза семейство 98 PF08307 Гликозилгидролаза семейство 98 C-концевой домен PF00457 Гликозилгидролазы семейство 11 PF00723 Гликозилгидролазы семейство 15 |
| PF00722 Гликозилгидролазы семейство 16 PF00332 Гликозилгидролазы семейство 17 PF00704 Гликозилгидролазы семейство 18 PF00703 Гликозилгидролазы семейство 2, иммуноглобулин-подобный бета-сэндвичевый домен PF02837 Гликозилгидролазы семейство 2, сахар-связывающий домен PF02836 Гликозилгидролазы семейство 2, TIM баррель-домен PF01183 Гликозилгидролазы семейство 25 PF00295 Гликозилгидролазы семейство 28 PF01055 Гликозилгидролазы семейство 31 PF08244 Гликозилгидролазы семейство 32 C-концевой PF00251 Гликозилгидролазы семейство 32 N-концевой PF01301 Гликозилгидролазы семейство 35 PF07748 Гликозилгидролазы семейство 38 C-концевой домен PF01074 Гликозилгидролазы семейство 38 N-концевой домен PF01229 Гликозилгидролазы семейство 39 PF04616 Гликозилгидролазы семейство 43 PF01341 Гликозилгидролазы семейство 6 PF01270 Гликозилгидролазы семейство 8 PF01630 Гиалуронидаза PF02922 Изоамилаза N-концевой домен |
| PF02435 Левансахараза/Инвертаза PF03200 Маннозилолигосахаридглюкозидаза PF02065 Мелибиаза PF08305 Домен NPCBM/NEW2 PF02927 N-концевой ig-подобный домен целлюлазы PF02055 O-Гликозилгидролаза семейство 30 PF07691 PA14-домен PF09113 Пептид-N-гликозидаза F, C-концевой PF09112 Пептид-N-гликозидаза F, N-концевой PF0l522 Полисахариддеацетилаза PF03173 Предполагаемый углевод-связывающий домен PF03173 Предполагаемый углевод-связывающий домен PF06204 Предполагаемый углевод-связывающий домен PF07944 Предполагаемая гликозилгидролаза неизвестной функции (DUF1680) PF03370 Предполагаемая фосфатаза регуляторная субъединица PF00686 Крахмал-связывающий домен |
||
| Деполимеризация угля | Clostridium Petrotoga Planctomycetaceae |
PF05448-Ацетилксиланэстераза (AXE1) PF01095-Пектинэстераза PF00135-Карбоксилэстераза Хелатазы Продуцирование низкомолекулярных органических кислот |
| Анаэробное (или аэробное) разложение полициклических ароматических углеводородов (PAH) | Thermoprotei Anaerovorax Smithella Anaerobaculum Thermacetogenium Aeromonas Dechloromonas Pseudomonas Thauera Marinobacter Alcanivorax Desulfuromonas Desulfovibrio Spirochaeta Azoarcus |
PF00067 Цитохром P450 PF00171 Семейство альдегиддегидрогеназы PF00775 Диоксигеназа PF00848 Альфа-субъединица гидроксилирования кольца (каталитический домен) PF00866 Бета-субъединица гидроксилирования кольца PF01188 Манделатрацемаза/муконатлактонизирующий фермент, C-концевой домен PF01231 Индоламин-2,3-диоксигеназа PF01361 Фермент таутомераза PF01596 O-метилтрансфераза PF01689 Гидратаза/декарбоксилаза PF01731 Арилэстераза PF01738 Семейство диенлактонгидролазы PF01869 Семейство BadF/BadG/BcrA/BcrD АТФазы PF01883 Домен неизвестной функции DUF59 PF02332 Метан/Фенол/Толуолгидроксилаза PF02426 Муконолактон дельта-изомераза PF02461 Аммиакмонооксигеназа PF02578 Неохарактеризованный ACR, YfiH семейство COG 1496 PF02626 Аллофанатгидролаза субъединица 2 PF02627 Семейство карбоксимуконолактондекарбоксилазы |
| PF02668 Диоксигеназа тауринового катаболизма TauD, семейство TfdA PF02746 Манделатрацемаза/муконатлактонизирующий фермент, N-концевой домен PF02798 Глутатион S-трансфераза, N-концевой домен PF02900 Каталитическая LigB субъединица диоксигеназы раскрытия ароматического кольца PF02962 5-Карбоксиметил-2-гидроксимуконатизомераза PF03079 Семейство ARD/ARD' PF03171 Суперсемейство 2OG-Fe(II) оксигеназы PF03241 Семейство 4-гидроксифенилацетат-3-гидроксилазы PF03301 Триптофан-2,3-диоксигеназа PF03349 Транспортный протеин наружного белка мембраны (OMPP1/FadL/TodX) PF03594 Протеин мембранного транспорта бензоата PF04209 Гомогентизат-1,2-диоксигеназа PF04303 Белок неизвестной функции (DUF453) PF04444 Пирокатехиндиоксигеназа N-конец PF04663 Фенолгидроксилаза консервативный участок PF04744 Монооксигеназа белок субъединицы B PF04896 Аммиакмонооксигеназа/метанмонооксигеназа, субъединица С |
| PF05145 Предполагаемая аммиакмонооксигеназа PF05494 Toluene tolerance Ttg2 PF05721 Фитаноил-CoA диоксигеназа (PhyH) PF05870 Фенольных кислот декарбоксилаза (PAD) PF06052 3-Гидроксиантраниловой кислоты диоксигеназа PF06099 Фенолгидроксилаза субъединица PF06234 Белок B системы толуол-4-монооксигеназы (TmoB) PF06917 Периплазматическая пектатлиаза PF07424 TrbM PF07746 Диоксигеназа раскрытия ароматических колец LigAB, LigA субъединица PF07976 Фенолгидроксилаза, C-концевой домен димеризации PF08201 Белок BssC/TutF PF08282 Галогенангидриддегалогеназа-подобная гидролаза PF08803 Предполагаемая монооксигеназа ydhR PF08883 Семейство Dopa 4,5-диоксигеназа PF09448 Метилмуконолактонметилизомераза PF09459 Этилбензолдегидрогеназа PF09662 Фенилфосфаткарбоксилаза гамма-субъединица (Phenyl_P gamma) |
||
| Гомоацетогенез | PF01268 Формилтетрагидрофолатсинтетаза PF03598 Комплекс CO дегидрогеназа/ацетил-CoA-синтаза бета- |
| субъединица PF03599 CO дегидрогеназа/ацетил-CoA синтаза дельта-субъединица |
||
| Метаногенез (гидрогено-трофный и ацетоклас-тический) | Methanothrix Methanosarcina Methanofolis Methanobacterium Methanolobus Methanocalculus Methanomicrobiales Methanocorposculum Methanosarcina |
PF01913 Формилметанофуран-тетрагидрометаноптеринформилтрансфераза PF01993 Метилентетрагидрометаноптериндегидрогеназа PF02007 Тетрагидрометаноптерин S-метилтрансфераза, H PF02240 Метил-кофермент M редуктаза гамма PF02241 Метил-кофермент M редуктаза бета-C-концевой PF02249 Метил-кофермент M редуктаза альфа C-концевой PF02289 Метенилтетрагидрометаноптеринциклогидролаза PF02505 Метил-кофермент M редуктазабелок D PF02663 Вольфрамформилметанофурандегидрогеназа, FwdE PF02741 Формилметанофуран-тетрагидрометаноптеринформилтрансфераза PF02745 Метил-кофермент M редуктаза альфа, N-концевой PF02783 Метил-кофермент M редуктаза бета-N-концевой PF04029 2-Фосфосульфолактатфосфатаза PF04206 Тетрагидрометаноптерин S-метилтрансфераза, E PF04207 Тетрагидрометаноптерин S-метилтрансфераза, D PF04208 Тетрагидрометаноптерин S-метилтрансфераза, A PF04210 Тетрагидрометаноптерин S-метилтрансфераза, G |
| PF04211 Тетрагидрометаноптерин S-метилтрансфераза, C PF04422 Кофермент F420 гидрогеназа бета-N-концевой PF04432 Кофермент F420 гидрогеназа, бета-C-концевой PF04609 Метил-кофермент M редуктаза белок C PF05440 Тетрагидрометаноптерин S-метилтрансфераза, B PF08979 Домен неизвестной функции (DUF1894) PF09176 Метилен-тетрагидрометаноптериндегидрогеназа, N-концевой PF09472 Тетрагидрометаноптерин S-метилтрансфераза, F |
Пример 3
Стимулирование продуцирования метана
Наличие определенного микробного сообщества, продуцирующего метан из угля in vitro, а также набора штаммов, способных осуществлять аэробное разложение угля, привело к проведению лабораторных экспериментов, в которых тестировали влияние различных стимуляторов на продуцирование метана. Фиг.13 показывает результаты стимуляции системы культур с различными количествами кислорода (2%, 4% и 10% O2) и электроноакцепторными сульфатом (при концентрациях 0,1 мМ, 1 мМ и 10 мМ) и нитратом (при концентрациях 0,1 мМ, 1 мМ и 10 мМ).
Наибольшее увеличение продуцирования метана наблюдали в ответ на кратковременные импульсные подачи кислорода, что позволяет предположить, что лимитирующим фактором продуцирования метана из угля может быть перенос электронов, создаваемый при аэробном разложении углеводородов. Это разложение стимулируется добавлением кислорода в качестве реактанта для ферментов классов оксигеназ, присутствующих в некоторых штаммах, входящих в DMA. Однако когда кислород вводят в количествах выше оптимальных уровней, он подавляет метаногенез, возможно, вследствие замены CO2 как концевого электроноакцептора и/или окисления чувствительных к кислороду ферментов либо в метан-продуцирующих бактериях, либо в других анаэробных группах микроорганизмов.
Приведенная ниже таблица 2 представляет список предполагаемых оксигеназ и соответствующих организмов-хозяев, идентифицированных методом 16S геномных анализов.
| ТАБЛИЦА 2 | |
| Предполагаемая оксигеназа | Предполагаемые организмы-хозяева |
| 2,3-дигидроксифенилпропионат-1,2-диоксигеназа | Bradyrhizobium sp. ORS278 |
| 2-нитропропандиоксигеназа, NPD | Alkaliphilus metalliredigens QYMF] |
| 20G-Fe(II) оксигеназа | Methylobacillus flagellatus KT] |
| 4-гидроксифенилпируват диоксигеназа | Pseudomonas aeuruginosa PA7] |
| Алкан-1-монооксигеназа | Pseudomonas mendocina ymp} |
| Монооксигеназа биосинтеза антибиотиков | Candidatus Desulfococcus oleovorans Hxd3] |
| Бензоат-1,2-диоксигеназа, альфа-субъединица | Burkholderia pseudomallei 668] |
| Диоксигеназа раскрытия ароматических колец | Pseudomonas entomophila L48] |
| Бифенил-2,3-диол-1,2 диоксигеназа III-родственный белок | Vibrio cholerae O1 biovar eltor str. N1696] |
| Каталитическая LigB субъединица диоксигеназы раскрытия ароматических колец | Leptospira borgpetersenii se rovar Hardjobovis L55] |
| Пирокатехин-2,3-диоксигеназа | Azoarcus sp. BH72] |
| Циклогексанонмонооксигеназа | Parvibaculum lavamentivorans DS-1] |
| Диоксигеназы, родственные 2-нитропропандиоксигеназе | Pseudomonas entomophila L48] |
| Дитерпеноиддиоксигеназа | Mycobacterium sp. JLS] |
| Диоксигеназа расщепления эстрадиольного кольца, фермент класса III, субъединица | Caldicellulosiruptor saccharolyticus DSM 8903] |
| Глиоксалаза/белок резистентности к блеомицину/диоксигеназа | Dechloromonas aromatica RCB] |
| Гомогентизат-1,2-диоксигеназа | Chromobacterium violaceum ATCC 12472] |
| Люциферазо-подобная монооксигеназа | Burkholderia mallei NCTC 10247] |
| Фенилацетат-CoA оксигеназа, субъединица PaaG | Burkholderia pseudomallei 1710b] |
| Вероятная диоксигеназа гидроксилирования кольца, субъединица | Pseudomonas aeruginosa PAO1] |
| Предполагаемая аммиакмонооксигеназа | Jannaschia sp. CCS1] |
| Предполагаемая диоксигеназа расщепления эстрадиольного кольца | Bradyrhizobium sp. BTAi1] |
| Предполагаемая протокатехат-3,4-диоксигеназа, белок бета-цепи | Vibrio parahae molyticus RIMD 2210633 |
| Толуат-1,2-диоксигеназа, компонент переноса электронов | Pseudomonas aeruginosa PA7] |
На фиг.4 приведено сравнение профиля монооксигеназ и диоксигеназ, обнаруженных при проведении 16S геномных анализов микроорганизмов пластовых вод, обогащенной метан-продуцирующей культуры, а также выделенных штаммов Pseudomonas и Thallasospira.
Добавление кислорода к DMA может привести к увеличению продуцирования метана только в тех случаях, когда это не оказывает влияния на строго анаэробных членов. Толерантность анаэробных бактерий и метаногенных архебактерий к кислороду была недавно описана (Boga, H.I. и Brune, A. 2003. Hydrogen-dependent oxygen reduction by homoacetogenic bacteria isolated from termite guts, Appl. Environ. Microbiol., 69: 779-786), и могут быть проведены испытания толерантности по отношению к кислороду чистой культуры, содержащей DMA.
Фиг.14 показывает увеличение продуцирования метана после стимуляции h2 и ацетатом в культурах, выращенных с использованием угля в качестве единственного источника углерода.
Фиг.15 демонстрирует увеличение продуцирования метана после стимуляции триметиламином в культурах, выращенных с использованием угля в качестве единственного источника углерода.
Все публикации и патентные заявки, приведенные в настоящем описании, включены в настоящее описание посредством ссылки в такой степени, как если бы каждая отдельная публикация и патентная заявка была конкретно и индивидуально указана, как включенная в качестве ссылки.
Claims (15)
1. Способ идентификации стимулятора, который повышает биогенное продуцирование метана в углеводородсодержащем пласте, где указанный способ включает:
(a) получение последовательности нуклеиновой кислоты от одного или более микроорганизмов, выделенных из среды углеводородсодержащего пласта;
(b) определение присутствия одного или более генных продуктов указанной последовательности нуклеиновой кислоты, где указанный генный продукт представляет собой фермент на пути метаболизма, вовлеченного в преобразование углеводорода в метан, выбранный из группы, состоящей из пероксидаз, фенолоксидаз, алкогольоксидаз, лакказ, гидролаз, гликозилгидролаз, эстераз, этераз, оксидаз, нитрогеназ, целлюлаз, амилаз, глюканаз, пуллуланаз, редуктаз, дисмутаз, оксигеназ, монооксигеназ, диоксигеназ, каталаз, гидрогеназ, карбоксилаз и метилредуктаз; или фермент, вовлеченный в гомоацетогенез, метаногенез, ацетокластический метаногенез или CO2-восстановительный метаногенез; и
(c) идентификацию субстрата, реактанта или кофактора указанного фермента, который повышает продуцирование метана, будучи доступным одному или более микроорганизмам в указанном углеводородсодержащем пласте, и
(d) идентификация тем самым стимулятора, который повышает биогенное продуцирование метана в углеводородсодержащем пласте по сравнению с продуцированном метана в углеводородсодержащем пласте в отсутствии стимулятора.
(a) получение последовательности нуклеиновой кислоты от одного или более микроорганизмов, выделенных из среды углеводородсодержащего пласта;
(b) определение присутствия одного или более генных продуктов указанной последовательности нуклеиновой кислоты, где указанный генный продукт представляет собой фермент на пути метаболизма, вовлеченного в преобразование углеводорода в метан, выбранный из группы, состоящей из пероксидаз, фенолоксидаз, алкогольоксидаз, лакказ, гидролаз, гликозилгидролаз, эстераз, этераз, оксидаз, нитрогеназ, целлюлаз, амилаз, глюканаз, пуллуланаз, редуктаз, дисмутаз, оксигеназ, монооксигеназ, диоксигеназ, каталаз, гидрогеназ, карбоксилаз и метилредуктаз; или фермент, вовлеченный в гомоацетогенез, метаногенез, ацетокластический метаногенез или CO2-восстановительный метаногенез; и
(c) идентификацию субстрата, реактанта или кофактора указанного фермента, который повышает продуцирование метана, будучи доступным одному или более микроорганизмам в указанном углеводородсодержащем пласте, и
(d) идентификация тем самым стимулятора, который повышает биогенное продуцирование метана в углеводородсодержащем пласте по сравнению с продуцированном метана в углеводородсодержащем пласте в отсутствии стимулятора.
2. Способ по п.1, который дополнительно включает улучшение одного или более микроорганизмов отбором на способность расти на угле в качестве единственного источника углерода.
3. Способ по п.1, в котором стадия (с) включает:
(i) тестирование in vitro одного или более субстратов, реактантов или кофакторов при более чем одной концентрации для мониторинга и оптимизации продуцирования метана в системе культур, включающей по меньшей мере один микроорганизм, выделенный из указанного углеводородсодержащего пласта, где дополнительно для указанной системы культур уголь является единственным источником углерода; или
(ii) тестирование in vitro одного или более субстратов, реактантов или кофакторов при более чем одной концентрации для мониторинга и оптимизации продуцирования метана в системе культур, включающей определенное микробное сообщество; где указанное определенное микробное сообщество сочетает культуру единичного штамма микроорганизма из углеводородсодержащего пласта по меньшей мере с одной другой определенной культурой еще одного единичного штамма микроорганизма, таким образом, что члены указанного определенного микробного сообщества проявляют синергическое действие в продуцировании метана; и где дополнительно для указанной системы культур уголь является единственным источником углерода.
(i) тестирование in vitro одного или более субстратов, реактантов или кофакторов при более чем одной концентрации для мониторинга и оптимизации продуцирования метана в системе культур, включающей по меньшей мере один микроорганизм, выделенный из указанного углеводородсодержащего пласта, где дополнительно для указанной системы культур уголь является единственным источником углерода; или
(ii) тестирование in vitro одного или более субстратов, реактантов или кофакторов при более чем одной концентрации для мониторинга и оптимизации продуцирования метана в системе культур, включающей определенное микробное сообщество; где указанное определенное микробное сообщество сочетает культуру единичного штамма микроорганизма из углеводородсодержащего пласта по меньшей мере с одной другой определенной культурой еще одного единичного штамма микроорганизма, таким образом, что члены указанного определенного микробного сообщества проявляют синергическое действие в продуцировании метана; и где дополнительно для указанной системы культур уголь является единственным источником углерода.
4. Способ по п.3, в котором указанный по меньшей мере один микроорганизм представляет собой вид бактерий, выбранных из группы родов, состоящей из Pseudomonas, Arcobacter, Desulfuromonas, Pelobacter, Desulfovibrio, Spirochaeta, Erysipelothrix, Thauera, Clostridium, Acholeplasma, Magneto spirillum и Sulfurospirillum; или вид архебактерий, выбранный из группы, состоящей из Methanolobus, Methanocalculus, и членов типа Crenarcheaota; или указанное определенное микробное сообщество включает по меньшей мере два вида микроорганизмов, выбранных из группы родов Pseudomonas, Arcobacter, Desulfuromonas, Pelobacter, Desulfovibrio, Spirochaeta, Erysipelothrix, Thauera, Clostridium, Acholeplasma, Magnetospirilium, Sulfurospirillum, Methanolobus, Methanocalculus, и членов типа Crenarcheaota.
5. Способ по п.1, в котором указанный углеводородсодержащий пласт выбирают из группы, состоящей из угля, торфа, бурого угля, битуминозного сланца, нефтеносного пласта, традиционных тяжелых нефтяных остатков, вязкой нефти, нефтеносных песков и битуминозных песков.
6. Способ по п.1, в котором указанный фермент выбирают из группы, состоящей из оксигеназ, монооксигеназ и диоксигеназ.
7. Способ по п.1, в котором указанные субстрат, реактант или кофактор выбирают из группы, состоящей из серосодержащего соединения, азотсодержащего соединения, фосфорсодержащего соединения, микроэлемента, электроноакцептора, электронодонора, галогена, металла, спирта, органической кислоты, алкана, алкена, алкина, ароматического соединения, амина, простого эфира, альдегида, кетона, тиола, ацетата, ароматического углеводорода и газа.
8. Способ повышения биогенного продуцирования метана в углеводородсодержащем пласте, включающий введение стимулятора, идентифицированного способом по п.1, в указанный углеводородсодержащий пласт.
9. Способ по п.8, где указанный способ включает введение кислорода в указанный углеводородсодержащий пласт.
10. Способ по п.9, где указанный углеводородсодержащий пласт представляет собой уголь.
11. Способ по п.8, дополнительно включающий модулирование фермента субстратом, реактантом или кофактором для повышения биогенного продуцирования метана в углеводородсодержащем пласте.
12. Способ по п.8, где углеводородсодержащий пласт, который представляет собой угольный пласт и скважины для добычи метана из угольных пластов, дополнительно включающий:
(d) получение культуры единичного штамма указанного одного или более микроорганизмов из указанной угольного пласта или скважины для добычи метана из угольных пластов, в которой единичный штамм микроорганизма содержит указанный один или более генных продуктов; и
(e) объединение указанного культивированного единичного штамма микроорганизма по меньшей мере с одной другой определенной культурой еще одного единичного штамма микроорганизма для получения определенного микробного сообщества; где члены указанного определенного микробного сообщества проявляют синергическое действие в продуцировании метана.
(d) получение культуры единичного штамма указанного одного или более микроорганизмов из указанной угольного пласта или скважины для добычи метана из угольных пластов, в которой единичный штамм микроорганизма содержит указанный один или более генных продуктов; и
(e) объединение указанного культивированного единичного штамма микроорганизма по меньшей мере с одной другой определенной культурой еще одного единичного штамма микроорганизма для получения определенного микробного сообщества; где члены указанного определенного микробного сообщества проявляют синергическое действие в продуцировании метана.
13. Способ по п.12, в котором указанное определенное микробное сообщество включает по меньшей мере два вида микроорганизмов, выбранных из группы родов, состоящей из Pseudomonas, Arcobacter; Desulfuromonas, Pelobacter, Desulfovibrio, Spirochaeta, Erysipelothrix, Thauera, Clostridium, Acholeplasma, Magnet о spirillum, Sulfurospirillum, Methanolobus, Methanocalculus, и членов типа Crenarcheaota.
14. Способ повышения биогенного продуцирования метана из угля, где указанный способ включает введение определенного микробного сообщества, идентифицированного способом по п.12, в угольный пласт.
15. Способ повышения биогенного продуцирования метана из угля, где указанный способ включает введение определенного микробного сообщества, идентифицированного способом по п.12, в угольный пласт вместе с указанным субстратом, реактантом или кофактором.
Applications Claiming Priority (3)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| US5262408P | 2008-05-12 | 2008-05-12 | |
| US61/052,624 | 2008-05-12 | ||
| PCT/US2009/043677 WO2009140313A1 (en) | 2008-05-12 | 2009-05-12 | Methods to stimulate biogenic methane production from hydrocarbon-bearing |
Publications (2)
| Publication Number | Publication Date |
|---|---|
| RU2010150769A RU2010150769A (ru) | 2012-06-20 |
| RU2488636C2 true RU2488636C2 (ru) | 2013-07-27 |
Family
ID=41319029
Family Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| RU2010150769/10A RU2488636C2 (ru) | 2008-05-12 | 2009-05-12 | Способы стимуляции биогенного продуцирования метана в углеводородсодержащих пластах |
Country Status (10)
| Country | Link |
|---|---|
| US (2) | US7977056B2 (ru) |
| EP (1) | EP2294281B1 (ru) |
| CN (1) | CN102027195B (ru) |
| AU (1) | AU2009246493B2 (ru) |
| BR (1) | BRPI0912617A2 (ru) |
| CA (1) | CA2724074C (ru) |
| PL (1) | PL220307B1 (ru) |
| RU (1) | RU2488636C2 (ru) |
| WO (1) | WO2009140313A1 (ru) |
| ZA (1) | ZA201007841B (ru) |
Cited By (1)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| US11578575B2 (en) | 2015-09-22 | 2023-02-14 | 9668241 Canada Inc. | Microbially enhanced thermal oil recovery |
Families Citing this family (57)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| US7426960B2 (en) | 2005-05-03 | 2008-09-23 | Luca Technologies, Inc. | Biogenic fuel gas generation in geologic hydrocarbon deposits |
| RU2488636C2 (ru) * | 2008-05-12 | 2013-07-27 | Синтетик Дженомикс, Инк. | Способы стимуляции биогенного продуцирования метана в углеводородсодержащих пластах |
| US8528634B2 (en) * | 2009-02-23 | 2013-09-10 | E.I. Du Pont De Nemours And Company | Method of improving oil recovery from an oil reservoir using an enriched anaerobic steady state microbial consortium |
| US20100216219A1 (en) * | 2009-02-23 | 2010-08-26 | E. I. Du Pont De Nemours And Company | Method of in situ bioremediation of hydrocarbon-contaminated sites using an enriched anaerobic steady state microbial consortium |
| US8753865B2 (en) * | 2009-02-23 | 2014-06-17 | E I Du Pont De Nemours And Company | Steady state anaerobic denitrifying consortium for application in in-situ bioremediation of hydrocarbon-contaminated sites and enhanced oil recovery |
| US8479813B2 (en) * | 2009-12-16 | 2013-07-09 | Luca Technologies, Inc. | Biogenic fuel gas generation in geologic hydrocarbon deposits |
| GB2488937B (en) * | 2009-12-24 | 2014-07-16 | Shell Int Research | In-situ microbial oxygen generation and hydrocarbon conversion in a hydrocarbon containing formation |
| FR2955335B1 (fr) * | 2010-01-19 | 2014-10-03 | Ecole Norm Superieure Lyon | Procede de production de gaz methane |
| WO2011153467A2 (en) * | 2010-06-04 | 2011-12-08 | Synthetic Genomics, Inc. | Methods to stimulate biogenic methane production from hydrocarbon-bearing formations |
| US10221432B2 (en) | 2010-06-16 | 2019-03-05 | Conocophillips Company | In situ methanogenesis modeling and risk analysis |
| US9376610B2 (en) * | 2010-11-01 | 2016-06-28 | E I Du Pont De Nemours And Company | Methods, strains, and compositions useful for microbially enhanced oil recovery: Arcobacter clade 1 |
| US20120295335A1 (en) * | 2010-11-18 | 2012-11-22 | E. I. Du Pont De Nemours And Company | Prevention of contamination of nutrient feed reservoirs & feed lines in bioreactor |
| WO2012135847A1 (en) * | 2011-03-31 | 2012-10-04 | University Of Wyoming | Biomass-enhanced natural gas from coal formations |
| US9376901B2 (en) | 2011-09-20 | 2016-06-28 | John Pantano | Increased resource recovery by inorganic and organic reactions and subsequent physical actions that modify properties of the subterranean formation which reduces produced water waste and increases resource utilization via stimulation of biogenic methane generation |
| US10577543B2 (en) * | 2011-10-27 | 2020-03-03 | Raymond Roger Wallage | Efficient oil shale recovery method |
| US9550943B2 (en) | 2011-10-27 | 2017-01-24 | Raymond Roger Wallage | Efficient oil shale recovery method |
| US9503512B2 (en) | 2012-03-21 | 2016-11-22 | Intertrust Technologies Corporation | Distributed computation systems and methods |
| US9004162B2 (en) * | 2012-03-23 | 2015-04-14 | Transworld Technologies Inc. | Methods of stimulating acetoclastic methanogenesis in subterranean deposits of carbonaceous material |
| MX2014015182A (es) * | 2012-06-27 | 2015-03-05 | Shell Int Research | Proceso y sistema de recuperacion de petroleo. |
| MX2014014777A (es) * | 2012-06-27 | 2015-02-24 | Shell Int Research | Proceso y sistema de recuperacion de petroleo. |
| MX2014014778A (es) * | 2012-06-27 | 2015-02-24 | Shell Int Research | Proceso y sistema de recuperacion de petroleo. |
| EP2694669B1 (en) | 2012-06-28 | 2017-05-17 | Taxon Biosciences, Inc. | Methods for making or creating a synthetic microbial consortium identified by computational analysis of amplicon sequences |
| CN103541702B (zh) * | 2012-07-12 | 2016-06-08 | 中国石油天然气股份有限公司 | 一种低渗透砂岩油藏提高原油采收率的方法 |
| US9090814B2 (en) | 2012-08-09 | 2015-07-28 | Baker Hughes Incorporated | Well treatment fluids containing an ylide or a vitamin B and methods of using the same |
| CN102900407B (zh) * | 2012-10-10 | 2016-02-10 | 中国石油化工股份有限公司 | 一种利用co2驱后油藏残余co2转化甲烷的方法 |
| CA2895154C (en) * | 2012-12-19 | 2021-02-16 | Commonwealth Scientific And Industrial Research Organisation | Nutrient composition, process and system for enhancing biogenic methane production from a carbonaceous material |
| JP2016513977A (ja) | 2013-03-14 | 2016-05-19 | ザ ユニバーシティ オブ ワイオミング リサーチ コーポレーション | 化学合成独立栄養細菌を利用した二酸化炭素の変換システムおよび方法 |
| US10557155B2 (en) | 2013-03-14 | 2020-02-11 | The University Of Wyoming Research Corporation | Methods and systems for biological coal-to-biofuels and bioproducts |
| KR20160026828A (ko) * | 2013-03-15 | 2016-03-09 | 시리스 에너지 인코포레이티드 | 탄소 함유 물질의 생물 전환 공정 |
| US20140299314A1 (en) * | 2013-04-05 | 2014-10-09 | Multi-Chem Group, Llc | Method for the use of nitrates and nitrate reducing bacteria for mitigating biogenic sulfide production |
| CA2911195A1 (en) * | 2013-04-05 | 2014-10-09 | Mo Bio Laboratories, Inc. | Kits and methods for isolating protein from biological and environmental samples |
| WO2014204849A1 (en) | 2013-06-18 | 2014-12-24 | Shell Oil Company | Oil recovery system and method |
| CA2915594A1 (en) | 2013-06-27 | 2014-12-31 | Shell Internationale Research Maatschappij B.V. | Remediation of asphaltene-induced plugging of wellbores and production lines |
| US20150075776A1 (en) * | 2013-07-24 | 2015-03-19 | D. Jack Adams | Optimization of biogenic methane production from hydrocarbon sources |
| WO2015031913A2 (en) * | 2013-08-30 | 2015-03-05 | Verliant Energy, Llc | System and method for improved anaerobic digestion |
| CN103670347B (zh) * | 2013-10-14 | 2017-01-04 | 华东理工大学 | 活化油藏中产甲烷菌转化二氧化碳生产甲烷的方法 |
| CN106103644B (zh) * | 2013-12-19 | 2018-11-23 | 联邦科学技术研究组织 | 在地下含碳介质中维持甲烷产生的方法 |
| CN105756637B (zh) * | 2014-12-19 | 2018-11-16 | 中国石油天然气股份有限公司 | 一种利用煤层有益内源微生物提高煤层气采收率的方法 |
| AU2016265999B1 (en) * | 2015-08-12 | 2017-02-23 | Commonwealth Scientific And Industrial Research Organisation | Methanogenesis |
| WO2017040992A1 (en) | 2015-09-04 | 2017-03-09 | Mo Bio Laboratories, Inc. | Methods for co-isolation of nucelic acids and proteins |
| US10597681B2 (en) | 2015-09-14 | 2020-03-24 | President And Fellows Of Harvard College | Carbon fixation systems and methods |
| EE201600003A (et) | 2016-02-16 | 2017-09-15 | Biotatec Oü | Meetod graptoliitargilliidi metallorgaanilise aine lõhustamiseks mikroobikoosluse abil |
| ES2904890T3 (es) | 2016-07-06 | 2022-04-06 | Harvard College | Métodos y sistemas para la síntesis de amoniaco |
| US11598194B1 (en) * | 2016-11-18 | 2023-03-07 | I.P. Co, Llc | Stimulation and continuous recovery of biogenic gas from coal beds |
| US20200102254A1 (en) * | 2017-05-17 | 2020-04-02 | President And Fellows Of Harvard College | Biofertilizer and methods of making and using same |
| CN111088967B (zh) * | 2018-10-24 | 2022-04-12 | 中国石油化工股份有限公司 | 一种提高油藏微生物产甲烷产量的方法 |
| CN110043234A (zh) * | 2019-04-04 | 2019-07-23 | 农业部沼气科学研究所 | 一种油泥沙处理方法及激活油泥沙微生物来提高原油采收率的方法 |
| JP7260904B2 (ja) * | 2019-04-15 | 2023-04-19 | アンヴァール株式会社 | バイオガスの生成方法 |
| CN110106155B (zh) * | 2019-05-28 | 2021-11-26 | 内蒙古科技大学 | 一种用于低阶煤炭生产清洁能源的复合酶制剂及制备方法 |
| CN110257291B (zh) * | 2019-06-25 | 2021-07-23 | 北京大学 | 一株耐受镍离子毒性的无色杆菌及其应用 |
| CN110805417B (zh) * | 2019-11-04 | 2021-09-24 | 中国石油化工股份有限公司 | 一种调控油藏内源微生物生长代谢规律的方法 |
| CN111100880A (zh) * | 2019-11-25 | 2020-05-05 | 浙江大学 | 磁小体促进微生物电发酵还原co2制备甲烷的方法 |
| JP7323881B2 (ja) * | 2020-03-09 | 2023-08-09 | 独立行政法人エネルギー・金属鉱物資源機構 | 炭化水素回収方法及び炭化水素回収システム |
| WO2022197698A1 (en) | 2021-03-15 | 2022-09-22 | University Of Wyoming | Methods for microbial gas production and use as an isotopic tracer |
| WO2022217117A1 (en) * | 2021-04-08 | 2022-10-13 | University Of Florida Research Foundation, Incorporated | Enzymatic synthesis of mycosporine-like amino acids |
| CN113738322B (zh) * | 2021-09-01 | 2022-04-26 | 中国矿业大学 | 一种利用产氢产乙酸菌改变煤渗透率的方法 |
| CN116064302B (zh) * | 2022-09-27 | 2024-03-01 | 福建农林大学 | 底部脱硫弧菌sg127及其应用 |
Citations (6)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| WO2001068904A1 (en) * | 2000-03-15 | 2001-09-20 | Exxonmobil Upstream Research Company | Process for stimulating microbial activity in a hydrocarbon-bearing, subterranean formation |
| WO2005113784A1 (en) * | 2004-05-12 | 2005-12-01 | Luca Technologies, Llc | Generation of hydrogen from hydrocarbon-bearing materials |
| WO2005115649A1 (en) * | 2004-05-28 | 2005-12-08 | University Of Newcastle Upon Tyne | Process for stimulating production of methane from petroleum in subterranean formations |
| WO2007082032A2 (en) * | 2006-01-11 | 2007-07-19 | Luca Technologies, Llc | Thermacetogenium phaeum consortium for the production of materials with enhanced hydrogen content |
| WO2007118094A2 (en) * | 2006-04-05 | 2007-10-18 | Luca Technologies, Inc. | Chemical amendments for the stimulation of biogenic gas generation in deposits of carbonaceous material |
| WO2007136716A2 (en) * | 2006-05-17 | 2007-11-29 | Green Earth Industries, Llc | Increased microbial production of methane gas from subsurface hydrocarbon containing formations |
Family Cites Families (4)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| US6156946A (en) * | 1996-04-12 | 2000-12-05 | Exxon Research And Engineering Company | Biological activation of aromatics for chemical processing and/or upgrading of aromatic compounds, petroleum, coal, resid, bitumen and other petrochemical streams |
| DE10335284B4 (de) * | 2003-07-28 | 2009-09-10 | Hueck Folien Gesellschaft M.B.H. | Vorrichtung zur Aufbewahrung von festen und/oder flüssigen und/oder gasförmigen Gegenständen |
| US7431083B2 (en) * | 2006-04-13 | 2008-10-07 | Schlumberger Technology Corporation | Sub-surface coalbed methane well enhancement through rapid oxidation |
| RU2488636C2 (ru) * | 2008-05-12 | 2013-07-27 | Синтетик Дженомикс, Инк. | Способы стимуляции биогенного продуцирования метана в углеводородсодержащих пластах |
-
2009
- 2009-05-12 RU RU2010150769/10A patent/RU2488636C2/ru active
- 2009-05-12 EP EP09747397.9A patent/EP2294281B1/en not_active Not-in-force
- 2009-05-12 CA CA2724074A patent/CA2724074C/en not_active Expired - Fee Related
- 2009-05-12 PL PL393466A patent/PL220307B1/pl unknown
- 2009-05-12 BR BRPI0912617A patent/BRPI0912617A2/pt not_active Application Discontinuation
- 2009-05-12 CN CN200980116909.0A patent/CN102027195B/zh not_active Expired - Fee Related
- 2009-05-12 WO PCT/US2009/043677 patent/WO2009140313A1/en active Application Filing
- 2009-05-12 AU AU2009246493A patent/AU2009246493B2/en not_active Ceased
- 2009-05-12 US US12/464,832 patent/US7977056B2/en not_active Expired - Fee Related
-
2010
- 2010-11-02 ZA ZA2010/07841A patent/ZA201007841B/en unknown
-
2011
- 2011-07-06 US US13/177,429 patent/US8448702B2/en not_active Expired - Fee Related
Patent Citations (6)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| WO2001068904A1 (en) * | 2000-03-15 | 2001-09-20 | Exxonmobil Upstream Research Company | Process for stimulating microbial activity in a hydrocarbon-bearing, subterranean formation |
| WO2005113784A1 (en) * | 2004-05-12 | 2005-12-01 | Luca Technologies, Llc | Generation of hydrogen from hydrocarbon-bearing materials |
| WO2005115649A1 (en) * | 2004-05-28 | 2005-12-08 | University Of Newcastle Upon Tyne | Process for stimulating production of methane from petroleum in subterranean formations |
| WO2007082032A2 (en) * | 2006-01-11 | 2007-07-19 | Luca Technologies, Llc | Thermacetogenium phaeum consortium for the production of materials with enhanced hydrogen content |
| WO2007118094A2 (en) * | 2006-04-05 | 2007-10-18 | Luca Technologies, Inc. | Chemical amendments for the stimulation of biogenic gas generation in deposits of carbonaceous material |
| WO2007136716A2 (en) * | 2006-05-17 | 2007-11-29 | Green Earth Industries, Llc | Increased microbial production of methane gas from subsurface hydrocarbon containing formations |
Non-Patent Citations (1)
| Title |
|---|
| YAVITT J.B. et al., Methanogenesis and methanogen diversity in peatlands of the discontinuous permafrost zone of Boreal western continental Canada, Geomicrobiology * |
Cited By (1)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| US11578575B2 (en) | 2015-09-22 | 2023-02-14 | 9668241 Canada Inc. | Microbially enhanced thermal oil recovery |
Also Published As
| Publication number | Publication date |
|---|---|
| EP2294281A1 (en) | 2011-03-16 |
| EP2294281B1 (en) | 2014-04-02 |
| EP2294281A4 (en) | 2011-09-14 |
| AU2009246493B2 (en) | 2014-01-23 |
| PL393466A1 (pl) | 2011-07-18 |
| RU2010150769A (ru) | 2012-06-20 |
| WO2009140313A1 (en) | 2009-11-19 |
| US20100047793A1 (en) | 2010-02-25 |
| CN102027195B (zh) | 2014-05-14 |
| US20110277991A1 (en) | 2011-11-17 |
| AU2009246493A1 (en) | 2009-11-19 |
| CA2724074A1 (en) | 2009-11-19 |
| WO2009140313A8 (en) | 2010-12-16 |
| AU2009246493A8 (en) | 2010-12-02 |
| ZA201007841B (en) | 2014-07-30 |
| BRPI0912617A2 (pt) | 2017-03-21 |
| US7977056B2 (en) | 2011-07-12 |
| CA2724074C (en) | 2016-04-12 |
| PL220307B1 (pl) | 2015-10-30 |
| CN102027195A (zh) | 2011-04-20 |
| US8448702B2 (en) | 2013-05-28 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| RU2488636C2 (ru) | Способы стимуляции биогенного продуцирования метана в углеводородсодержащих пластах | |
| Park et al. | Biogenic methane production from coal: a review on recent research and development on microbially enhanced coalbed methane (MECBM) | |
| US10358660B2 (en) | Compositions and methods for identifying and modifying carbonaceous compositions | |
| CN1988970B (zh) | 刺激从地层石油产生甲烷的方法 | |
| Siegert et al. | Starting up microbial enhanced oil recovery | |
| Guo et al. | Important role of fungi in the production of secondary biogenic coalbed methane in China’s Southern Qinshui Basin | |
| Rathi et al. | Evaluating the potential of indigenous methanogenic consortium for enhanced oil and gas recovery from high temperature depleted oil reservoir | |
| WO2011089151A2 (fr) | Procede de production de gaz methane | |
| AU2011261306B2 (en) | Methods to stimulate biogenic methane production from hydrocarbon-bearing formations | |
| Dong et al. | Biostimulation of biogas producing microcosm for enhancing oil recovery in low-permeability oil reservoir | |
| Ameen | Uses of Microorganisms in The Recovery of Oil and Gas | |
| Mukherjee et al. | New insights into the coal-associated methane architect: the ancient archaebacteria | |
| Schweitzer et al. | Effect of an algal amendment on the microbial conversion of coal to methane at different sulfate concentrations from the Powder River Basin, USA | |
| Kotlar et al. | Use of petroleum biotechnology throughout the value chain of an oil company: an integrated approach | |
| DZ et al. | YS 000k |