JP2014207909A - マイクロ−rnaスキャホールドおよび非天然存在型マイクロ−rna - Google Patents
マイクロ−rnaスキャホールドおよび非天然存在型マイクロ−rna Download PDFInfo
- Publication number
- JP2014207909A JP2014207909A JP2014116024A JP2014116024A JP2014207909A JP 2014207909 A JP2014207909 A JP 2014207909A JP 2014116024 A JP2014116024 A JP 2014116024A JP 2014116024 A JP2014116024 A JP 2014116024A JP 2014207909 A JP2014207909 A JP 2014207909A
- Authority
- JP
- Japan
- Prior art keywords
- mir
- hsa
- mirna
- sequence
- mature
- Prior art date
- Legal status (The legal status is an assumption and is not a legal conclusion. Google has not performed a legal analysis and makes no representation as to the accuracy of the status listed.)
- Pending
Links
Images
Classifications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/11—DNA or RNA fragments; Modified forms thereof; Non-coding nucleic acids having a biological activity
- C12N15/113—Non-coding nucleic acids modulating the expression of genes, e.g. antisense oligonucleotides; Antisense DNA or RNA; Triplex- forming oligonucleotides; Catalytic nucleic acids, e.g. ribozymes; Nucleic acids used in co-suppression or gene silencing
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61P—SPECIFIC THERAPEUTIC ACTIVITY OF CHEMICAL COMPOUNDS OR MEDICINAL PREPARATIONS
- A61P43/00—Drugs for specific purposes, not provided for in groups A61P1/00-A61P41/00
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/11—DNA or RNA fragments; Modified forms thereof; Non-coding nucleic acids having a biological activity
- C12N15/111—General methods applicable to biologically active non-coding nucleic acids
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6869—Methods for sequencing
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2310/00—Structure or type of the nucleic acid
- C12N2310/10—Type of nucleic acid
- C12N2310/14—Type of nucleic acid interfering N.A.
- C12N2310/141—MicroRNAs, miRNAs
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2310/00—Structure or type of the nucleic acid
- C12N2310/50—Physical structure
- C12N2310/53—Physical structure partially self-complementary or closed
- C12N2310/531—Stem-loop; Hairpin
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2320/00—Applications; Uses
- C12N2320/30—Special therapeutic applications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2330/00—Production
- C12N2330/30—Production chemically synthesised
Landscapes
- Health & Medical Sciences (AREA)
- Life Sciences & Earth Sciences (AREA)
- Engineering & Computer Science (AREA)
- Genetics & Genomics (AREA)
- Chemical & Material Sciences (AREA)
- Biomedical Technology (AREA)
- Organic Chemistry (AREA)
- Zoology (AREA)
- Wood Science & Technology (AREA)
- Bioinformatics & Cheminformatics (AREA)
- General Engineering & Computer Science (AREA)
- Biotechnology (AREA)
- Molecular Biology (AREA)
- General Health & Medical Sciences (AREA)
- Biochemistry (AREA)
- Microbiology (AREA)
- Physics & Mathematics (AREA)
- Biophysics (AREA)
- Proteomics, Peptides & Aminoacids (AREA)
- Plant Pathology (AREA)
- Analytical Chemistry (AREA)
- Immunology (AREA)
- Medicinal Chemistry (AREA)
- Public Health (AREA)
- Animal Behavior & Ethology (AREA)
- General Chemical & Material Sciences (AREA)
- Pharmacology & Pharmacy (AREA)
- Chemical Kinetics & Catalysis (AREA)
- Nuclear Medicine, Radiotherapy & Molecular Imaging (AREA)
- Veterinary Medicine (AREA)
- Micro-Organisms Or Cultivation Processes Thereof (AREA)
- Pharmaceuticals Containing Other Organic And Inorganic Compounds (AREA)
- Medicines That Contain Protein Lipid Enzymes And Other Medicines (AREA)
- Measuring Or Testing Involving Enzymes Or Micro-Organisms (AREA)
- Medicines Containing Material From Animals Or Micro-Organisms (AREA)
Abstract
【課題】遺伝子ノックダウンを効果的に媒介する非天然存在型miRNA類を形成するためにターゲット配列類を統合できるmiRNA系スキャホールド類を提供する。【解決手段】miR−196a−2またはmiR−204などの第1の内在性miRNAに由来するスキャホールド、第2の内在性miRNAに由来する成熟鎖、および、前記熟成鎖の配列に少なくとも一部相補的であるスター鎖配列からなる、幹−ループ構造を有する非天然存在型miRNA。また、miR−196a−2またはmiR−204などの内在性miRNAに由来するスキャホールド、標的RNAに少なくとも一部相補的であるように設計した成熟鎖、および、前記熟成鎖配列に少なくとも一部相補的であるスター鎖配列からなる、幹−ループ構造を有する非天然存在型miRNA。さらに、RNAi経路による遺伝子サイレンシングを媒体する方法および組成物。【選択図】図2
Description
本願は、米国特許仮出願番号第60/939,785(出願日:2007年5月23日)に基づいて優先権を主張するものであり、前記出願のすべての記載をここに引用するものである。
本発明はRNAiの分野に係り、特に、遺伝子ノックダウンを効果的に媒介する非天然存在型miRNA類を形成するためにターゲット配列類を統合できるmiRNA系スキャホールド類に係る。
RNA干渉(RNAi)は、転写後の遺伝子修飾に必要な、ほぼ偏在的な経路である。RNAiの鍵となる重要な分子は、マイクロRNA(以後、miRNAまたはmiRと呼ぶ)である。これら小さな、非コードRNA類は、プライマリーmiRNA類(以後、pri−RNAと呼ぶ)として転写され、pre−miRNA類と呼ばれる短いヘアピン構造を形成するために、Drosha(タイプIII リボヌクレアーゼ)により核内で処理される(図1参照)。こうして得られた分子は、チトプラズムに運搬され、RNA誘発サイレンシング複合体(RISC)に組み込まれる前に第2のヌクレアーゼ(Dicer)によって処理される。成熟miRNA−RISC複合体とメッセンジャーRNA(mRNA)との干渉、特に、miRNAガイド鎖のシード領域(ヌクレオチド2位−7位)とmRNAの3’UTR領域との干渉は、転写切断および/または翻訳能減衰により遺伝子ノックダウンを引き起こす。
近年、固有の基質(miRNA)への研究がかなりの興味を集めてきた一方で、RNAi経路も強力な研究手段として認識されてきた。合成化学または酵素的方法により生成した小さな2本鎖RNA類(以後、小さな干渉RNAまたはsiRNAと呼ぶ)を、脂質媒介型トランスフェクションやエレクトロポレーションなどの様々な手段により細胞内に導入し、分解させるために、特定の遺伝子転写を標的にすることができる。このように、RNAi経路は、遺伝子機能、経路分析、および医薬品の発見を研究する上で重要な手段として役立つものであり、さらに、将来は治療薬としての適用も考えられている。
Grimm,D,(2006)、Nature Letters 441:537−541)
合成siRNAの利用は、ほとんどの遺伝子ノックダウン実験が必要とすることに役立つにもかかわらず、合成分子が適当ではない事例もある。少数の細胞タイプには、通常用いるトランスフェクション法および/または試薬類が効かないタイプや、または、非常に鋭敏過ぎるタイプがある。さらに別の例では、実験系の必要性から、合成分子が供給される期間(典型的には4−10日間)よりも長い期間をかけて遺伝子ノックダウンが達成されることが求められる。
サイレンシング試薬のベクター系による輸送は、レンチウイルスなどによる輸送および単純なヘパリンやmiRNA系スキャホールド構造体を用いることで過去成し遂げられてきた。非特許文献1参照。
本発明は、第1の内在性miRNAに由来するスキャホールド、第2の内在性miRNAに由来する成熟鎖、この成熟鎖配列に少なくとも一部相補的なスター鎖配列を有する幹−ループ構造をもつ非天然存在型miRNAを提供する。
また、本発明は、幹−ループ構造の幹が成熟鎖−スター鎖2本鎖を組み込んだ幹−ループ構造をもつ核酸からなる非天然存在型miR−196a−2miRNAを提供する。成熟鎖の配列は、成熟内在性miRNAに由来するが、しかし、miR−196a−2の内在性成熟鎖の配列とは全く異なる。スター鎖は、成熟鎖に少なくとも一部相補的である。いくつかの実施形態では、成熟鎖は、19ヌクレオチド長から25ヌクレオチド長の間の長さをもつ。また、ある実施形態では、成熟鎖の1位にあるヌクレオチドはUである。また、ある実施形態では、成熟鎖の12位にあるヌクレオチドは、スター鎖上の相対する位置にあるヌクレオチドと塩基対を生成しない。
また、本発明は、幹−ループ構造の幹が成熟鎖−スター鎖2本鎖を組み込んだ幹−ループ構造をもつ核酸からなる非天然存在型miR−204−miRNAを提供する。成熟鎖の配列は成熟内在性miRNAに由来するが、しかし、miR−204の内在性成熟鎖の配列とは全く異なる。スター鎖は、成熟鎖に少なくとも一部相補的である。
また、本発明は、成熟内在性miRNAとほぼ同等な成熟miRNAを生成するために、細胞内で処理され得る非天然存在型miR−196a−2miRNAを提供する。なお、前記成熟内在性miRNAの配列は、内在性miR−196a−2成熟miRNAの配列とは異なる。
また、本発明は、成熟内在性miRNAとほぼ同等な成熟miRNAを生成するために、細胞内で処理され得る非天然存在型miR−204miRNAを提供する。なお、前記成熟内在性miRNAの配列は、内在性miR−204成熟miRNAの配列とは異なる。
また、本発明は、内在性miRNA(例えば、miR−196a−2またはmiR−204)に由来するスキャホールド、標的RNAに少なくとも一部相補的(例えば、成熟鎖の2位−7位が標的RNAに相補的であるような)ではあるが内在性miRNA成熟鎖とは異なる成熟鎖、および、前記成熟鎖配列と少なくとも一部相補的であるスター鎖配列とを有する幹−ループ構造をもつ非天然存在型miRNAを提供する。
また、本発明は、非天然存在型miRNA類、例えば、非天然存在型miR−196a−2 miRNAまたは非天然存在型miR−204 miRNAを有する細胞を提供する。
また、本発明は、細胞内の標的RNAの機能を低下させる方法を提供する。この方法には、非天然存在型miRNA(例えば、非天然存在型miR−196a−2 miRNAまたは非天然存在型miR−204 miRNA)を発現可能なベクターに、細胞を接触する工程が含まれる。前記非天然存在型miRNAは、内在性miRNAにほぼ同等なmiRNAを生成するために細胞内で処理される。
また、本発明は、非天然存在型miRNA(例えば、非天然存在型miR−196a−2 miRNAまたは非天然存在型miR−204 miRNA)をコードするヌクレオチド類配列を有するリコンビナント発現ベクター類を提供する。
本発明は、非天然存在型miRNA(例えば、非天然存在型miR−196a−2 miRNAまたは非天然存在型miR−204 miRNA)を有し、さらに、少なくとも一つの薬学的に許容なキャリアを有する薬学的組成物を提供する。
さらに、本発明は、ある遺伝子が不適当に発現するのを特徴とする疾患を治療する医薬品の製造に、非天然存在型miRNA(例えば、非天然存在型miR−196a−2 miRNAまたは非天然存在型miR−204 miRNA)を使用する方法を開示する。ここで、前記遺伝子は、前記非天然存在型miRNAによって標的にされる。
本発明の他の態様をここに開示する。
「人工イントロン」という用語は、イントロンとして作用するように設計された特定の配列を意味する。
「合理的設計」という用語は、高い機能性レベルで遺伝子サイレンシングを提供する配列が同定される可能性を増す条件一式を使用する設計方法を意味する。
「レポーター」または「レポーター遺伝子」という用語は、発現を観察できる遺伝子を意味する。例えば、レポーターの発現レベルは、RNAi経路の基質によって遺伝子サイレンシングが成功したかどうか調べるために評価することが可能である。
「RNA誘発サイレンシング複合体」およびその頭字語「RISC」という用語は、切断、翻訳減衰、メチル化、および/または他の変形を行うためにmRNAなどの核酸分子類を標的にするため、成熟miRNAまたはsiRNAなどの単鎖ポリヌクレオチドと複合体を作るタンパク質一式を意味する。RISCの、既に知られた限定されない構成要素には、siRNA類やmiRNA類とともに、Dicer、R2D2、およびArugonauteタンパク質ファミリーが含まれる。
「RNA干渉」および「RNAi」という用語は同義語であり、ポリリボヌクレオチド単位を少なくとも1つ含むポリヌクレオチド(miRNAまたはsiRNA)が、生物学的プロセスに影響を及ぼすプロセスを意味する。このプロセスは、補助タンパク質を用いたDNAのメチル化とともに、mRNA分解、翻訳減衰、tRNA、rRNA、hnRNA、およびゲノムDNAとの相互作用による遺伝子サイレンシングを含むが、これらに限定されるものではない。
「遺伝子サイレンシング」という用語は、特定の遺伝子産物の発現がRNA干渉により減少するまたは減衰するプロセスを意味する。遺伝子サイレンシングレベル(時には、「ノックダウン」の程度とも称されるが)は、様々な手段により測定できるが、その手段としては、ノーザンブロット分析法による転写レベルの測定、B−DNA技術、転写感受性レポ−ター、発現プロファイリング(例えば、DNAチップ)、qRT−PCR、および関連技術が含まれるが、これらに限定されるものではない。他方、サイレンシングレベルは、特定遺伝子によってコードされるタンパク質のレベルを調べることで測定できる。この方法は、ウエスタン分析法、蛍光タンパク質(GFPなど)をもつレポータータンパク質の発現レベルの測定、または酵素活性(例えば、アルカリホスファターゼ)、またはその他の方法を含む、数多くの研究を行うことで実施できる。
「マイクロRNA」、「miRNA」、または「miR」という用語は全て、RNAi経路に入ることが可能であり、遺伝子発現を調節できる非コードRNA類を意味するが、これらのRNA類をコードするDNA配列類をも意味する。「プライマリーmiRNA」または「pri−miRNA」は、Droshaプロセス前の非コード転写を表し、フランキング5’配列および3’配列とともに、幹−ループ配列を含む。「プレカーサーmiRNA」または「pre−miRNA」は、pri−miRNAのDroshaプロセス後の非コード転写を表す。「成熟miRNA」という用語は、pre−miRNAのDicerプロセスによって得られる2本鎖産物を意味するか、または、Dicerプロセスに続きRISKに導入される単鎖産物を意味する。ある場合には、miRNAの単鎖だけがRNAi経路に入る。また、別の場合には、miRNAの2本鎖がRNAi経路に入ることができる。
「成熟鎖」という用語は、内在性miRNA中の配列を意味するか、または、所望の標的RNAの完全または一部逆相補的(RC)である非天然存在型miRNAを意味する。「成熟配列」、「標的鎖」、「標的配列」、および「ガイド鎖」の用語は、「成熟鎖」という用語と同義であり、しばしば交換可能に用いられる。
「スター鎖」という用語は、miRNA中の成熟鎖に完全または一部相補的である鎖を意味する。「パッセンジャー鎖」および「スター鎖」という用語は、交換可能である。
「標的配列」という用語は、成熟鎖と一部または完全に相補的である、標的RNA中またはDNA中の配列を意味する。標的配列は、DNAの4つの塩基(A、T、G、およびC)、またはRNAの4つの塩基(A、U、G、およびC)、を用いて記載することができる。ある場合には、標的配列は内在性miRNA成熟鎖により認識される配列である。別の場合には、標的配列はランダムに決定される。またある場合には、標的配列は、1つ以上の所望の特徴に基づいて好ましい標的配列類を同定するアルゴリズムによって同定することができる。
「標的RNA」という用語は、RNAの機能活性を減少させるRNAi経路によって標的となる特定のRNAを意味する。ある場合には、RNA標的は、翻訳能がその機能であるmRNAである。また、ある場合には、RNAi経路により、翻訳減衰または切断を通してmRNAの機能活性が減少する。本発明では、標的RNA類は非天然存在型miRNA類により標的にされる。「標的」という用語は、DNAも意味する。
「内在性miRNA」という用語は、生物のゲノム内に本来存在する配列の転写により、その生物内で生産されるmiRNAを意味する。内在性miRNAは、例えば、イントロン、オープンリーディングフレーム(ORF)、5’または3’非翻訳領域(UTR)、または、遺伝子間領域の中に局在可能である。内在性miRNAを生産する生物は、ヒト(または他の霊長類)、マウス、ラット、ハエ、虫類、魚類、または完全なRNAi経路をもつ他の生物であってよいが、これらに限定されるものではない。
「相補的」という用語は、互いに塩基対を形成するためにポリヌクレオチドがもつ傾向を意味する。非平行なポリヌクレオチド鎖の中にあるヌクレオチド単位どうしの間に、一般に水素結合により塩基対が形成される。相補的ポリヌクレオチド鎖は、ワトソン−クリック様式(例えば、A対T、A対U、C対G)で塩基対を形成できる。または、UとGの間に形成されるゆらぎ塩基対を含む、2本鎖を形成可能ないかなる様式でも塩基対を形成できる。当業者が知るように、DNAに対してRNAを用いる場合、チミンよりもウラシルの方がアデノシンに相補的な塩基と考えられる。本発明の中でUが示された場合、他に説明がない限りTを置換できることを意味する。
完全相補性、または100%相補性という用語は、1つのポリヌクレオチド鎖の各ヌクレオチド単位が、第2のポリヌクレオチド鎖のヌクレオチド単位と水素結合できる状態を意味する。部分相補性とは、2本の鎖の、全部ではないがいくつかのヌクレオチド単位が、互いに水素結合できる状態を意味する。例えば、少なくとも6塩基対−7塩基対が約19−25ヌクレオチド長に対して形成される時、2本の鎖は少なくとも部分相補的である。また、各配列が他の配列に対して(部分または完全)逆相補的(RC)である時、配列類は互いに「相補的」であると称される。例えば、配列5’GATC3’は、その逆相補的配列3’ CTAG5’に対して完全相補的である。また、配列類はゆらぎ塩基対をもつこともできる。
「2本鎖」という用語は、互いに塩基対を形成する、2本の相補的またはほぼ相補的ポリヌクレオチドにより形成される2本鎖構造を意味する。ワトソン−クリック塩基対やU−Gゆらぎ塩基対が含まれ、少なくとも部分相補的であるポリヌクレオチド鎖間の2本鎖構造を安定化する。2本鎖である鎖は、2本鎖を形成するために必ずしも完全相補的である必要はない。例えば、1つ以上のミスマッチを2本鎖は有してもよい。
単ポリヌクレオチド分子は、分子内塩基対をもつ2本鎖を形成しうる非平行で相補的なポリヌクレオチド鎖を有することができる。このようなポリヌクレオチド類は、しばしば幹−ループ構造を有する。幹−ループ構造では、幹の鎖類は主に単鎖であるループ配列によって分離され、完全に非平行な配置をとることができる。幹−ループ構造は、この技術分野においてよく知られている。Pre−miRNA類およびPri−miRNA類は、しばしば、幹が成熟鎖−スター鎖2本鎖を有する1つ以上の幹−ループ構造をもつ。
「ヌクレオチド」という用語は、リボヌクレオチドまたはデオキシリボヌクレオチドまたは、それらを修飾した形を意味するとともに、その誘導体を意味する。ヌクレオチドは、アデニン、ハイポキサンチン、グアニン、およびその誘導体や類縁体などのプリン類、チトシン、ウラシシル、チミン、およびその誘導体や類縁体などのピリミジン類からなる構成要素を有する。ヌクレオチド類縁体には、塩基、糖および/またはホスフェートの化学構造を修飾したヌクレオチドを含む。これらの修飾には、5位ピリミジン修飾、8位プリン修飾、チトシン エキソサイクリックアミン修飾、5−ブロモウラシルを含むが、これに限定されるものではない。さらに、2’位糖の修飾も含まれるが、2’−OHが、H、OR、R,ハロゲン、SH、SR、NH2、NHR、NR2またはCNなどの基で置換され、Rがアルキル基である、糖修飾リボヌクレオチドも含まれるが、これらに限定されるものではない。また、ヌクレオチド類縁体は、イノシン、クエウオシン、キサンチンなどの塩基類、2’メチルリボースなどの糖類、イネチルホスホネート、ホスホチオエートおよびペプチドなどの非天然型ホスホジエステル結合部類をもつヌクレオチド類を含むことも意味する。
修飾塩基という用語は、アデニン、グアニン、チトシン、チミン、ウラシル、キサンチン、イノシン、およびクエウオシンなどの塩基が、1つ以上の原子または基で置換または付加して修飾されているヌクレオチド塩基を意味する。塩基部分が修飾されているヌクレオチドを含む修飾例としては、アルキル化、ハロゲン化、チオール化、アニノ化、アミド化、アセチル化で修飾された塩基類が挙げられるが、単独またはこれらの組み合わせでもよい。さらに具体的な例としては、5−プロピニルウリジン、5−プロピニルシチジン、6−メチルアデニン、6−メチルグアニン、N,N−ジメチルアデニン、2−プロピルアデニン、2−プロピルグアニン、2−アミノアデニン、1−メチルイノシン、3−メチルウリジン、5−メチルシチジン、5−メチルウリジン、および5位が修飾されたその他のヌクレオチド類、5−(2−アミノ)プロピル ウリジン、5−ハロシチジン、5−ハロウリジン、4−アセチルシチジン、1−メチルアデノシン、2−メチルアデノシン、3−メチルシチジン、6−メチルウリジン、2−メチルグアノシン、7−メチルグアノシン、2,2−ジメチルグアノシン、5−メチルアミノエチルウリジン、5−メチルオキシウリジン、7−デアザ−アデノシン、6−アゾウリジン、6−アゾシチジン、6−アゾチミジン、5−メチル−2−チオウリジン、などのデアザヌクレオチド類、2−チオウリジン、4−チオウリジン、2−チオシチジン、ジヒドロウリジン、シュードウリジン、クエウオシン、アルカエオシンなどのその他のチオ塩基類、ナフチルおよび置換ナフチル基、N6−メチルアデノシン、5−メチルカルボニルメチルウリジン、ウリジン5−オキシ酢酸、ピリジン−4−オン、ピリジン−2−オンなどのO−およびN−アルキル化プリン類およびピリミジン類、アミノフェノールまたは2,4,6−トリメトキシベンゼンなどのフェニルおよび修飾フェニル基、G−クランプヌクレオチドとして働く修飾チトシン類、8−置換アデニン類およびグアニン類、5−置換ウラシル類およびチミン類、アザピリミジン類、カルボキシヒドロキシアルキル ヌクレオチド類、カルボキシアルキルアミノヌクレオチド類、およびアルキルカルボニルアルキル化ヌクレオチド類が挙げられる。また、修飾ヌクレオチドには、糖部分が修飾されたヌクレオチドも含まれるとともに、リボースではない糖または糖類縁体をもつヌクレオチドも含まれる。例えば、この糖部分は、マンノース、アラビノース、グルコピラノース、ガラクトピラノース、4’−チオリボース、およびその他の糖類、複素環または炭素環であってよい。
ヌクレオチドという用語は、本技術分野で一般的に知られた塩基も含むことも意味する。例えば、3−ニトロピロール、5−ニトロインドール、またはネブラリンなどの一般的塩基を含むが、これに限定されるものではない。また、「ヌクレオチド」という用語は、リボシル3’酸素をアミノ基で置換した、N3’−P5’ホスホラミダイトを含む。さらに、「ヌクレオチド」という用語には、ヌクレオチドに放射活性、蛍光またはマスラベルなどの検出可能な標識をもつものも含まれる。
「ポリヌクレオチド」という用語は、2つ以上のヌクレオチドからなるポリマー類を意味し、DNA、RNA、DNA/RNAハイブリッドを含むが、これらに限定されるものではない。DNA、RNA、DNA/RNAハイブリッドは、デオキシリボシル部分およびリボシル部分を規則的および/または不規則に変換したポリヌクレオチド鎖を有する。これらの変換されたヌクレオチド単位類は、糖部分の2’位に、−OH、続いて−H、続いて−OH、続いて−Hなどをもつ。さらに、DNA、RNA、DNA/RNAハイブリッドは、任意の位置のヌクレオチド単位類に様々な部分構造を取り付けた、この種のポリヌクレオチド類を修飾したものも含むが、これらに限定されるものではない。
「リボヌクレオチド」および「リボ核酸(RNA)」という用語は、少なくとも1つのリボヌクレオチド単位をもつ、修飾または無修飾のヌクレオチドまたはポリヌクレオチドを意味する。リボヌクレオチド単位は、リボシル部分1’位のN−グリコシド結合部に結合した窒素含有塩基をもつリボシル部分2’位に結合した水酸基を有し、別のヌクレオチドに結合できるかまたは結合を不可能にする部分構造を有する。
一様態として、本発明は、標的RNAの機能を低下できる非天然存在型miRNA(人工miRNAとも称する)を提供する。「非天然存在型miRNA」(ここでは、特定の内在性miRNAを意味する)は、特定の内在性miRNA由来の幹−ループ構造を有するpre−miRNAまたはpri−miRNAを意味する。この特定の内在性miRNAでは、幹−ループ構造の幹が成熟鎖−スター鎖2本鎖を導入するが、この2本鎖中では成熟鎖配列は特定の内在性miRNAの内在性成熟鎖配列とは異なるものである。また、本発明の非天然存在型miRNAのスター鎖配列も、特定の内在性miRNAの内在性成熟鎖配列とは異なるものである。
成熟鎖−スター鎖2本鎖の外部にある非天然存在型miRNAの配列類(例えば、以下に詳述するようにフランキング配列を含んでもよい成熟鎖−スター鎖2本鎖のどちらか一方にあるループおよび幹領域)を、ここでは「miRNAスキャホールド」、「スキャホールドタンパク」または単に「スキャホールド」と称する。従って、別の様態では、本発明は非天然存在型miRNAを生産するのに有用なmiRNAスキャホールドを提供する。本発明の非天然存在型miRNAは、特定の内在性miRNA由来の(例えば、少なくとも60%一致から100%一致を含む)miRNAスキャホール)を有し、さらに、前記特定の内在性miRNAからは得られない成熟鎖−スター鎖2本鎖を有する。本発明の、単一miRNAスキャホールドは、ほぼ限りない数の異なる非天然存在型miRNA類を提供することに利用できる。それぞれの非天然存在型miRNAは、同じmiRNA配列を有するが、異なる成熟鎖およびスター鎖配列を有する。
ここで、「非天然存在型miRNA」という用語は、RNA分子だけではなく、ある文脈ではこのRNA分子をコードするDNA分子を含むことを、当業者は認めるであろう。
本発明のmiRNAスキャホールド配列が由来する内在性miRNA類としては、ヒト由来のmiR−26b、miR−196a−2、およびmiR−204(miRNA Accession No.MIMAT0000083,MIMAT0000226,MIMAT0000265。それぞれ、http://microrna.sanger.ac.uk/sequences/index.shtmlより入手可能)、および、他の種由来のmiR−26b、miR−196a−2、およびmiR−204が含まれるが、これらに限定されるものではない。この説明の中では、2つのmiRNAは、各配列の成熟鎖が一致またはほぼ一致する場合に、同等であると判定する。従って、「非天然存在型miR−196a−2miRNA」という用語は、(例えば、miR−196a−2または同等の配列由来のmiRNAスキャホールドなどの)miR−196a−2miRNAを有し、さらに、内在性miR−196a−2の内在性成熟鎖およびスター鎖とは異なる内在性成熟鎖およびスター鎖を有する、pre−miRNAまたはpri−miRNAを意味する。従って、非天然存在型miR−196a−2miRNAは、miR−196a−2(任意の種)由来の幹−ループ構造を有する。このmiR−196a−2では、幹−ループ構造の幹は、成熟鎖配列がmiR−196a−2の内在性成熟鎖配列とは異なる、成熟鎖−スター鎖2本鎖を組み込んでいる。同様に、「非天然存在型miR−204 miRNA」という用語は、miR−204スキャホールド(例えば、miR−204由来のmiRNAスキャホールド)およびmiR−204由来ではない成熟鎖−スター鎖配列を有する、pre−miRNAまたはpri−miRNAを意味する。非天然存在型miR−204 miRNAは、miR−204(任意の種)由来の幹−ループ構造を有する。このmiR−204では、幹−ループ構造の幹は、成熟鎖配列がmiR−204の内在性成熟鎖配列とは異なる、成熟鎖−スター鎖2本鎖を組み込んでいる。
miRNAスキャホールド配列は、具体的に述べた内在性miRNA(例えば、miR−196a−2またはmiR−204)と同じものであってよい。また、miRNAスキャホールド配列は、内在性miRNA配列について1つ以上のヌクレオチドを付加、置換、または除去するという点で、具体的に述べた内在性miRNAとは異なっていてもよい。このような修飾、例えば、制限領域を導入することによって、miRNAスキャホールドの機能を高めることができる。制限領域は、miRNAスキャホールドに成熟鎖−スター鎖配列を導入することで、さらに、細胞内で発現するように非天然存在型miRNAをベクターに導入することで、クローニング戦略を助長することができる。また、成熟鎖およびスター鎖の長さを短縮するために、および、効率的かつ特定遺伝子サイレンシング能を生み出すために、ヌクレオチド変換をmiRNAスキャホールド内で行うことができる。また、RISCと相互作用して、得られた非天然存在型miRNA内のスター鎖機能を最小にするために、miRNAスキャホールドに対して配列修飾を行うことができる。また別の例では、miRNAスキャホールドのループに存在するヌクレオチドの数を、製造効率を改善するために減らすことができる。
miRNAスキャホールドは、さらに5’および/または3’フランキング配列を有してもよい(例えば、pre−miRNAを生産するためにDroshaで先ず処置したpri−miRNAとして、非天然存在型miRNAを提供することが望ましい場合)。このようなフランキング配列類は、幹ループの5’および/または3’末端を側面に置き、約5ヌクレオチド長から約600ヌクレオチド長、好ましくは、約5ヌクレオチド長から約150ヌクレオチド長の長さで並べられる。フランキング配列は、内在性miRNAの幹−ループ構造の5’および/または3’末端を側面に置く。miRNAスキャホールドはこの内在性miRNAに由来するか、または、1つ以上の塩基対が付加、除去または置換されて異なっていてもよい。たとえば、miR−196a−2miRNAスキャホールド(および成熟鎖配列およびスター鎖配列をクローニングすることにより得られる、非天然存在型miR−196a−2miRNA)は、内在性miR−196a−2miRNAの幹−ループ構造の5’および/または3’末端を側面に置く内在性配列類と同じ、5’および/または3’フランキング配列を有してもよい。
5’および/または3’フランキング配列類は、具体的に述べたmiRNA以外は、内在性miRNAの幹−ループ構造の5’および/または3’末端を側面に置く内在性配列類から得ることができる。例えば、いくつかの実施形態では、miR−196a−2miRNAスキャホールドは、miR−204などの別のmiRNAの幹−ループ構造の5’および/または3’末端を側面に置く内在性配列類に由来する、5’および/または3’フランキング配列類を有する。また、別の例では、5’および/または3’フランキング配列類は、miRNAの折りたたみ、処理過程、または機能性に最小の影響しか及ぼさないように設計または証明された人工的な配列類であてよい。また、別の例では、5’および/または3’フランキング配列類は、Drosha、Dicer、またはRNAi経路の他の構成要素によって、非天然存在型miRNAの折りたたみまたは処理過程を増強する、またはそれを妨げることのない天然配列類である。また、成熟miRNAを生産するために、非天然存在型miRNAの処理過程を増強する1つ以上のヌクレオチドモチーフおよび/または2次構造をもつように、フランキング配列類を設計または選択することができる。従って、例えば、非天然存在型miRNAが発現目的のためにイントロン内に埋め込まれる場合、発現遺伝子から非天然存在型miRNAの切り出しを増強する切断ドナーまたはアクセプターサイトを有するように、miRNAスキャホールド内のフランキング配列類を修飾可能である。一方、特有な配列または配列類によってmiRNA処理過程を増強する場合には、このような配列類を5’および/または3’フランキング配列内に挿入することが可能である。こうした配列類は、AUに富んだ配列類、およびRNAiマシナリーの1つ以上の構成要素と親和性をもつ配列類、およびRNAiマシナリーによって処理過程を増強する2次構造を形成させる配列類を有してもよい。ある実施形態では、フランキング配列は、図4に示されるように人工イントロンを有する。
また、別の実施形態では、miRNAスキャホールド内にある5’および/または3’フランキング配列類を、miRNAスキャホールドの他の部分の種とは異なる種から得てもよい。例えば、miR−196a−2 miRNAスキャホールド内にある5’および/または3’フランキング配列類を、ラットmiR−196a−2フランキング領域(または、他のラットmiRNAのフランキング領域)から得てもよい。しかし一方では、miR−196a−2 miRNAスキャホールドの残りの部分は、ヒトmiR−196a−2から得られる。
本発明のmiRNAスキャホールド類は、1)明確な幹およびループ構造をもち、2)最小の2次構造をもち、クローニングを促進するように修飾可能であり、3)非天然存在型miRNAがPol IIまたはPol IIIプロモーターから発現されるようにさせ、5)ループの大きさと配列を変換可能であり、6)非天然存在型miRNAがプラスミドとしてエピジェネティクス的に保持される時、またはホストゲノムに挿入される時に、非天然存在型miRNAを機能するようにさせ、7)非天然存在型miRNAを生産するために、内在性成熟miRNA配列の位置に、外部配列類を挿入または置換することが可能である。前記スキャホールドが、GFPなどのレポ−ター遺伝子またはプロマイシンなどの選択可能な標識遺伝子、またはその両者に関係する場合は、好適なmiRNAスキャホールド類は、5’UTR、3’UTR、イントロン配列または前記遺伝子のORFに挿入されても、機能することができる。好適な例では、GFPをコードする遺伝子をもつ融合構築体は、2つのコード配列および前記融合構築体の3’UTR内に挿入した人工miRNA−196a−2を機能的に分離する、Peptide 2Aをコードする配列をプロマイシンにコードする遺伝子に対し、機能的に融合される。図6(f)および図6(g)は、miR−204およびmiR−196a−2スキャホールドの非限定的例をそれぞれ示す。成熟鎖およびスター鎖を挿入するサイトが図示される。内在性miR−204およびmiR−196a−2に関するヌクレオチド類の置換は、ここにあるフォーマットを用いて示される。このような置換では、クローニングを促進するために限定領域を導入する。
上記で記載したように、本発明の非天然存在型miRNAは、特定内在性miRNAから得られるmiRNAスキャホールドを有し、さらに前記特定内在性miRNAからは得られない成熟鎖−スター鎖2本鎖を有する。本発明の非天然存在型miRNAの成熟鎖は、前記スキャホールドが得られる内在性miRNAと同じ長さにすることができるが、長くも短くもすることができる。また、本発明の非天然存在型miRNAの成熟鎖の長さは、得られた非天然存在型miRNAがDroshaおよび/またはDicerにより処置することができれば、その長さは重要ではない。
本発明の非天然存在型miRNAの成熟鎖のヌクレオチド配列は、1)他の内在性miRNAと同じものであるか、または他の内在性miRNAから得ることが可能であり、2)標的mRNA配列に基づいて選択する、または、3)標的mRNA配列に基づいて合理的に選択することができる。以下に、成熟鎖のこれら3種の原料について説明する。
<別の内在性miRNA(shMIMICS)から成熟鎖を得る実施形態>
最初の実施形態では、非天然存在型miRNAのmiRNAスキャホールド部分が由来するmiRNAとは全く異なる、別の内在性miRNAの成熟鎖配列(例えば、少なくとも60%同等から100%同等な配列)に、非天然存在型miRNAの配列が由来するものである。このような非天然存在型miRNAを「shMIMIC」と称することとする。このようなshMIMIC類は、第1の内在性miRNAから得られるスキャホールド、第2の内在性miRNAから得られる成熟鎖、および前記成熟鎖配列に少なくとも部分的に相補的であるスター鎖をもつ、幹−ループ構造を有する。
最初の実施形態では、非天然存在型miRNAのmiRNAスキャホールド部分が由来するmiRNAとは全く異なる、別の内在性miRNAの成熟鎖配列(例えば、少なくとも60%同等から100%同等な配列)に、非天然存在型miRNAの配列が由来するものである。このような非天然存在型miRNAを「shMIMIC」と称することとする。このようなshMIMIC類は、第1の内在性miRNAから得られるスキャホールド、第2の内在性miRNAから得られる成熟鎖、および前記成熟鎖配列に少なくとも部分的に相補的であるスター鎖をもつ、幹−ループ構造を有する。
例えば、miRNA−196a−2 shMIMICは、miRNA−196a−2由来のmiRNAスキャホールド構造をもつが、miRNA−196a−2以外の内在性miRNAの成熟鎖由来の成熟鎖も有する。好ましくは、miRNA−196a−2 shMIMICの成熟鎖配列は、約18から約23個の長さのヌクレオチド類、例えば、18、19、20、21、22、23個の長さのヌクレオチド類である。しかし、成熟鎖配列の長さは、shMIMICがDroshaやDicerにより認識され処理される限り、重要ではない。従って、18ヌクレオチド長より短い成熟鎖配列、および23ヌクレオチド長よりも長い成熟鎖配列を、miR−196a−2スキャホールド内に収めてもよい。miR−196a−2スキャホールドに基づいた、shMIMIC類の一般的な設計概念を、図11に示す。
ある一連の実施形態では、miRNA−196a−2 shMIMICは、ホモサピエンス(hsa)由来の、以下に示す任意のmiRNA類の成熟鎖配列に由来した成熟鎖配列を有する。hsa-let-7a-l, hsa-let-7a-2, hsa-let-7a-3, hsa-let-7b, hsa-let-7c, hsa-let-7d, hsa-let-7e, hsa-let-7f-l, hsa-let-7f-2, hsa-let-7g, hsa-let-7i, hsa-mir-1-1, hsa-mir-1-2, hsa-mir-7-1, hsa-mir-7-2, hsa-mir-7-3, hsa-mir-9-1, hsa-mir-9-2, hsa-mir-9-3, hsa-mir-10a, hsa-mir-10b, hsa-mir-15a, hsa-mir-15b, hsa-mir-16-1, hsa-mir-16-2, hsa-mir-17, hsa-mir-18a, hsa-mir-18b, hsa-mir-19a, hsa-mir-19b-l, hsa-mir-19b-2, hsa-mir-20a, hsa-mir-20b, hsa-mir-21, hsa-mir-22, hsa-mir-23a, hsa-mir-23b, hsa-mir-24-1, hsa-mir-24-2, hsa-mir-25, hsa-mir-26a-l, hsa-mir-26a-2, hsa-mir-26b, hsa-mir-27a, hsa-mir-27b, hsa-mir-28, hsa-mir-29a, hsa-mir-29b-l, hsa-mir-29b-2, hsa-mir-29c, hsa-mir-30a, hsa-mir-30b, hsa-mir-30c-l, hsa-mir-30c-2, hsa-mir-30d, hsa-mir-30e, hsa-mir-31, hsa-mir-32, hsa-mir-33a, hsa-mir-33b, hsa-mir-34a, hsa-mir-34b, hsa-mir-34c, hsa-mir-92a-l, hsa-mir-92a-2, hsa-mir-92b, hsa-mir-93, hsa-mir-95, hsa-mir-96, hsa-mir-98, hsa-mir-99a, hsa-mir-99b, hsa-mir-100, hsa-mir-101-1, hsa-mir-101-2, hsa-mir-103-1, hsa-mir-103-2, hsa-mir-105-1, hsa-mir-105-2, hsa-mir-106a, hsa-mir-106b, hsa-mir-107, hsa-mir-122, hsa-mir-124-1, hsa-mir-124-2, hsa-mir-124-3, hsa-mir-125a, hsa-mir-125b-l, hsa-mir-125b-2, hsa-mir-126, hsa-mir-127, hsa-mir-128-1, hsa-mir-128-2, hsa-mir-129-1, hsa-mir-129-2, hsa-mir-130a, hsa-mir-130b, hsa-mir-132, hsa-mir-133a- 1, hsa-mir-133a-2, hsa-mir-133b, hsa-mir-134, hsa-mir-135a-l, hsa-mir-135a-2, hsa-mir-135b, hsa-mir-136, hsa-mir-137, hsa-mir-138-1, hsa-mir-138-2, hsa-mir-139, hsa-mir-140, hsa-mir-141, hsa-mir-142, hsa-mir-143, hsa-mir-144, hsa-mir-145, hsa-mir-146a, hsa-mir-146b, hsa-mir-147, hsa-mir-147b, hsa-mir-148a, hsa-mir-148b, hsa-mir-149, hsa-mir-150, hsa-mir-151, hsa-mir-152, hsa-mir-153-1, hsa-mir-153-2, hsa-mir-154, hsa-mir-155, hsa-mir-181a-l, hsa-mir-181a-2, hsa-mir-181b-1, hsa-mir-181b-2, hsa-mir-181c, hsa-mir-181d, hsa-mir-182, hsa-mir-183, hsa-mir-184, hsa-mir-185, hsa-mir-186, hsa-mir-187, hsa-mir-188, hsa-mir-190, hsa-mir-190b, hsa-mir-191, hsa-mir-192, hsa-mir-193a, hsa-mir-193b, hsa-mir-194-1, hsa-mir-194-2, hsa-mir-195, hsa-mir-196a-1, hsa-mir-196b, hsa-mir-197, hsa-mir-198, hsa-mir-199a-1, hsa-mir-199a-2, hsa-mir-199b, hsa-mir-200a, hsa-mir-200b, hsa-mir-200c, hsa-mir-202, hsa-mir-203, hsa-mir-204, hsa-mir-205, hsa-mir-206, hsa-mir-208a, hsa-mir-208b, hsa-mir-210, hsa-mir-211, hsa-mir-212, hsa-mir-214, hsa-mir-215, hsa-mir-216a, hsa-mir-216b, hsa-mir-217, hsa-mir-218-1, hsa-mir-218-2, hsa-mir-219-1, hsa-mir-219-2, hsa-mir-220a, hsa-mir-220b, hsa-mir-220c, hsa-mir-221, hsa-mir-222, hsa-mir-223, hsa-mir-224, hsa-mir-296, hsa-mir-297, hsa-mir-298, hsa-mir-299, hsa-mir-300, hsa-mir-301a, hsa-mir-301b, hsa-mir-302a, hsa-mir-302b, hsa-mir-302c, hsa-mir-302d, hsa-mir-302e, hsa-mir-302f, hsa-mir-320a, hsa-mir-320b-1, hsa-mir-320b-2, hsa-mir-320c-l, hsa-mir-320c-2, hsa-mir-320d-l, hsa-mir-320d-2, hsa-mir-323, hsa-mir-324, hsa-mir-325, hsa-mir-326, hsa-mir-328, hsa-mir-329-1, hsa-mir-329-2, hsa-mir-330, hsa-mir-331, hsa-mir-335, hsa-mir-337, hsa-mir-338, hsa-mir-339, hsa-mir-340, hsa-mir-342, hsa-mir-345, hsa-mir-346, hsa-mir-361, hsa-mir-362, hsa-mir-363, hsa-mir-365-1, hsa-mir-365-2, hsa-mir-367, hsa-mir-369, hsa-mir-370, hsa-mir-371, hsa-mir-372, hsa-mir-373, hsa-mir-374a, hsa-mir-374b, hsa-mir-375, hsa-mir-376a-l, hsa-mir-376a-2, hsa-mir-376b, hsa-mir-376c, hsa-mir-377, hsa-mir-378, hsa-mir-379, hsa-mir-380, hsa-mir-381, hsa-mir-382, hsa-mir-383, hsa-mir-384, hsa-mir-409, hsa-mir-410, hsa-mir-411, hsa-mir-412, hsa-mir-421, hsa-mir-422a, hsa-mir-423, hsa-mir-424, hsa-mir-425, hsa-mir-429, hsa-mir-431, hsa-mir-432, hsa-mir-433, hsa-mir-448, hsa-mir-449a, hsa-mir-449b, hsa-mir-450a-l, hsa-mir-450a-2, hsa-mir-450b, hsa-mir-451, hsa-mir-452, hsa-mir-453, hsa-mir-454, hsa-mir-455, hsa-mir-483, hsa-mir-484, hsa-mir-485, hsa-mir-486, hsa-mir-487a, hsa-mir-487b, hsa-mir-488, hsa-mir-489, hsa-mir-490, hsa-mir-491, hsa-mir-492, hsa-mir-493, hsa-mir-494, hsa-mir-495, hsa-mir-496, hsa-mir-497, hsa-mir-498, hsa-mir-499, hsa-mir-500, hsa-mir-501, hsa-mir-502, hsa-mir-503, hsa-mir-504, hsa-mir-505, hsa-mir-506, hsa-mir-507, hsa-mir-508, hsa-mir-509-1, hsa-mir-509-2, hsa-mir-509-3, hsa-mir-510, hsa-mir-511-1, hsa-mir-511-2, hsa-mir-512-1, hsa-mir-512-2, hsa-mir-513a-l, hsa-mir-513a-2, hsa-mir-513b, hsa-mir-513c, hsa-mir-514-1, hsa-mir-514-2, hsa-mir-514-3, hsa-mir-515-1, hsa-mir-515-2, hsa-mir-516a-1, hsa-mir-516a-2, hsa-mir-516b-1, hsa-mir-516b-2, hsa-mir-517a, hsa-mir-517b, hsa-mir-517c, hsa-mir-518a-1, hsa-mir-518a-2, hsa-mir-518b, hsa-mir-518c, hsa-mir-518d, hsa-mir-518e, hsa-mir-518f, hsa-mir-519a-1, hsa-mir-519a-2, hsa-mir-519b, hsa-mir-519c, hsa-mir-519d, hsa-mir-519e, hsa-mir-520a, hsa-mir-520b, hsa-mir-520c, hsa-mir-520d, hsa-mir-520e, hsa-mir-520f, hsa-mir-520g, hsa-mir-520h, hsa-mir-521-1, hsa-mir-521-2, hsa-mir-522, hsa-mir-523, hsa-mir-524, hsa-mir-525, hsa-mir-526a-l, hsa-mir-526a-2, hsa-mir-526b, hsa-mir-527, hsa-mir-532, hsa-mir-539, hsa-mir-541, hsa-mir-542, hsa-mir-543, hsa-mir-544, hsa-mir-545, hsa-mir-548a-l, hsa-mir-548a-2, hsa-mir-548a-3, hsa-mir-548b, hsa-mir-548c, hsa-mir-548d-l, hsa-mir-548d-2, hsa-mir-548e, hsa-mir-548f-l, hsa-mir-548f-2, hsa-mir-548f-3, hsa-mir-548f-4, hsa-mir-548f-5, hsa-mir-548g, hsa-mir-548h-l, hsa-mir-548h-2, hsa-mir-548h-3, hsa-mir-548h-4, hsa-mir-548i-l, hsa-mir-548i-2, hsa-mir-548i-3, hsa-mir-548i-4, hsa-mir-548j, hsa-mir-548k, hsa-mir-5481, hsa-mir-548m, hsa-mir-548n, hsa-mir-548o, hsa-mir-548p, hsa-mir-549, hsa-mir-550-1, hsa-rair-550-2, hsa-mir-551a, hsa-mir-551b, hsa-mir-552, hsa-mir-553, hsa-mir-554, hsa-mir-555, hsa-mir-556, hsa-mir-557, hsa-mir-558, hsa-mir-559, hsa-mir-561, hsa-mir-562, hsa-mir-563, hsa-mir-564, hsa-mir-566, hsa-mir-567, hsa-mir-568, hsa-mir-569, hsa-mir-570, hsa-mir-571, hsa-mir-572, hsa-mir-573, hsa-mir-574, hsa-mir-575, hsa-mir-576, hsa-mir-577, hsa-mir-578, hsa-mir-579, hsa-mir-580, hsa-mir-581, hsa-mir-582, hsa-mir-583, hsa-mir-584, hsa-mir-585, hsa-mir-586, hsa-mir-587, hsa-mir-588, hsa-mir-589, hsa-mir-590, hsa-mir-591, hsa-mir-592, hsa-mir-593, hsa-mir-595, hsa-mir-596, hsa-mir-597, hsa-mir-598, hsa-mir-599, hsa-mir-600, hsa-mir-601, hsa-mir-602, hsa-mir-603, hsa-mir-604, hsa-mir-605, hsa-mir-606, hsa-mir-607, hsa-mir-608, hsa-mir-609, hsa-mir-610, hsa-mir-611, hsa-mir-612, hsa-mir-613, hsa-mir-614, hsa-mir-615, hsa-mir-616, hsa-mir-617, hsa-mir-618, hsa-mir-619, hsa-mir-620, hsa-mir-621 , hsa-mir-622, hsa-mir-623 , hsa-mir-624, hsa-mir-625, hsa-mir-626, hsa-mir-627, hsa-mir-628, hsa-mir-629, hsa-mir-630, hsa-mir-631, hsa-mir-632, hsa-mir-633, hsa-mir-634, hsa-mir-635, hsa-mir-636, hsa-mir-637, hsa-mir-638, hsa-mir-639, hsa-mir-640, hsa-mir-641, hsa-mir-642, hsa-mir-643, hsa-mir-644, hsa-mir-645, hsa-mir-646, hsa-mir-647, hsa-mir-648, hsa-mir-649, hsa-mir-650, hsa-mir-651, hsa-mir-652, hsa-mir-653, hsa-mir-654, hsa-mir-655, hsa-mir-656, hsa-mir-657, hsa-mir-658, hsa-mir-659, hsa-mir-660, hsa-mir-661, hsa-mir-662, hsa-mir-663, hsa-mir-663b, hsa-mir-664, hsa-mir-665, hsa-mir-668, hsa-mir-671, hsa-mir-675, hsa-mir-708, hsa-mir-720, hsa-mir-744, hsa-mir-758, hsa-mir-760, hsa-mir-765, hsa-mir-766, hsa-mir-767, hsa-mir-768, hsa-mir-769, hsa-mir-770, hsa-mir-802, hsa-mir-873, hsa-mir-874, hsa-mir-875, hsa-mir-876, hsa-mir-877, hsa-mir-885, hsa-mir-886, hsa-mir-887, hsa-mir-888, hsa-mir-889, hsa-mir-890, hsa-mir-891a, hsa-mir-891b, hsa-mir-892a, hsa-mir-892b, hsa-mir-920, hsa-mir-921, hsa-mir-922, hsa-mir-923, hsa-mir-924, hsa-mir-933, hsa-mir-934, hsa-mir-935, hsa-mir-936, hsa-mir-937, hsa-mir-938, hsa-mir-939, hsa-mir-940, hsa-mir-941-1, hsa-mir-941-2, hsa-mir-941-3, hsa-mir-941-4, hsa-mir-942, hsa-mir-943, hsa-mir-944, hsa-mir-1178, hsa-mir-1179, hsa-mir-1180, hsa-mir-1181, hsa-mir-1182, hsa-mir-1183, hsa-mir-1184, hsa-mir-1185-1, hsa-mir-1185-2, hsa-mir-1197, hsa-mir-1200, hsa-mir-1201, hsa-mir-1202, hsa-mir-1203, hsa-mir-1204, hsa-mir-1205, hsa-mir-1206, hsa-mir-1207, hsa-mir-1208, hsa-mir-1224, hsa-mir-1225, hsa-mir-1226, hsa-mir-1227, hsa-mir-1228, hsa-mir-1229, hsa-mir-1231, hsa-mir-1233, hsa-mir-1234, hsa-mir-1236, hsa-mir-1237, hsa-mir-1238, hsa-mir-1243, hsa-mir-1244, hsa-mir-1245, hsa-mir-1246, hsa-mir-1247, hsa-mir-1248, hsa-mir-1249, hsa-mir-1250, hsa-mir-1251, hsa-mir-1252, hsa-mir-1253, hsa-mir-1254, hsa-mir-1255a, hsa-mir-1255b-l, hsa-mir-1255b-2, hsa-mir-1256, hsa-mir-1257, hsa-mir-1258, hsa-mir-1259, hsa-mir-1260, hsa-mir-1261, hsa-mir-1262, hsa-mir-1263, hsa-mir-1264, hsa-mir-1265, hsa-mir-1266, hsa-mir-1267, hsa-mir-1268, hsa-mir-1269, hsa-mir-1270, hsa-mir-1271, hsa-mir-1272, hsa-mir-1273, hsa-mir-1274a, hsa-mir-1274b, hsa-mir-1275, hsa-mir-1276, hsa-mir-1277, hsa-mir-1278, hsa-mir-1279, hsa-mir-1280, hsa-mir-1281, hsa-mir-1282, hsa-mir-1283-1, hsa-mir-1283-2, hsa-mir-1284, hsa-mir-1285-1, hsa-mir-1285-2, hsa-mir-1286, hsa-mir-1287, hsa-mir-1288, hsa-mir-1289-1, hsa-mir-1289-2, hsa-mir-1290, hsa-mir-1291, hsa-mir-1292, hsa-mir-1293, hsa-mir-1294, hsa-mir-1295, hsa-mir-1296, hsa-mir-1297, hsa-mir-1298, hsa-mir-1299, hsa-mir-1300, hsa-mir-1301, hsa-mir-1302-1, hsa-mir-1302-2, hsa-mir-1302-3, hsa-mir-1302-4, hsa-mir-1302-5, hsa-mir-1302-6, hsa-mir-1302-7, hsa-mir-1302-8, hsa-mir-1303, hsa-mir-1304, hsa-mir-1305, hsa-mir-1306, hsa-mir-1307, hsa-mir-1308, hsa-mir-1321, hsa-mir-1322, hsa-mir-1323, hsa-mir-1324, hsa-mir-1825, hsa-mir-1826, または、hsa-mir-1827。
同様に、miRNA−204 shMIMICは、miRNA−204由来のmiRNAスキャホールド構造をもつが、miRNA−204以外(miRNA−196a−2および前段落に記載した任意のmiR類を含む)の内在性miRNAの成熟鎖由来の成熟鎖も有する。
shMIMICの成熟鎖配列は、内在性配列と同じでよい。または、特定のmiRNAスキャホールド内の成熟鎖の機能活性を最適にするために、shMIMICの成熟鎖配列を内在性配列に関して修飾してもよい。例えば、miRNA−196a−2スキャホールドを用いて効率的に標的化を行うために、成熟鎖1位にはUが好ましいことを本発明者は見出した。miRNA−196a−2スキャホールドに挿入する成熟鎖が、1位にU以外のヌクレオチドを有する場合、Uが第1位に存在するようにこの配列を変換することが好適である。理論や作用機構に拘らず、成熟鎖類は、2位から7位にかけて標的miRNAを分離すると思われる。この理由から、shMIMIC内にある特定のmiRNAの成熟鎖1位を変換しても、miRNAの標的特異性が変わる可能性はない。
shMIMICのスター鎖は、ほとんどの部分で成熟鎖の逆相補鎖であるが、スキャホールドが由来するmiRNAの内在性成熟鎖−スター鎖2本鎖構造をミミックするように局所構造を変換することが好ましい。miRNA−196a−2 shMIMIC用のスター鎖の特徴には、図3に示し、以下に詳細を述べるように、次にあげる特徴が1つ以上含まれることが好ましい。
1.成熟鎖1位がUである時(上で説明したように、好適であるが必須条件ではない)、スター鎖の相対する位置は、ゆらぎ塩基対となるようにGが好適である。
2.成熟鎖5位がGまたはT(U)の場合、スター鎖の相対する位置は、ゆらぎ塩基対となるようにT(U)またはGにそれぞれ変換することが好適である。
3.成熟鎖が5位にGまたはT以外の塩基をもつ場合、スター鎖の相対する位置は、標準的なワトソン−クリック塩基対をなすように設計することが好適である。
4.成熟鎖12位とスター鎖の相対する位置との間には、ミスマッチが形成されることが好適である。ミスマッチ形成は、スター鎖の相対する位置が成熟鎖12位と同じ塩基をもつことで達成される。
5.成熟鎖の長さが18ヌクレオチド長またはそれ以上の場合、成熟鎖5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟18位およびスター鎖の相対する位置に同様に適用される。特に、成熟鎖18位がGまたはT(U)の場合、スター鎖の相対する位置は、ゆらぎ塩基対となるようにT(U)またはGにそれぞれ変換される。成熟鎖が18位にGまたはT(U)以外の塩基をもつ場合は、スター鎖の相対する位置は、標準的なワトソン−クリック塩基対を形成するように設計する。
6.成熟鎖の長さが19ヌクレオチド長またはそれ以上の場合、成熟鎖5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟19位およびスター鎖の相対する位置に、同様に適用される。特に、成熟鎖19位がGまたはT(U)の場合、スター鎖の相対する位置は、ゆらぎ塩基対となるようにT(U)またはGにそれぞれ変換される。成熟鎖が19位にGまたはT(U)以外の塩基をもつ場合は、スター鎖は、標準的なワトソン−クリック塩基対を形成するように設計する。
7.成熟鎖の長さが21ヌクレオチド長またはそれ以上の場合、成熟鎖5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟21位およびスター鎖の相対する位置に、同様に適用される。特に、成熟鎖21位がGまたはT(U)の場合、スター鎖の相対する位置は、ゆらぎ塩基対となるようにT(U)またはGにそれぞれ変換される。成熟鎖が21位にGまたはT(U)以外の塩基をもつ場合は、スター鎖は、標準的なワトソン−クリック塩基対を形成するように設計する。
1.成熟鎖1位がUである時(上で説明したように、好適であるが必須条件ではない)、スター鎖の相対する位置は、ゆらぎ塩基対となるようにGが好適である。
2.成熟鎖5位がGまたはT(U)の場合、スター鎖の相対する位置は、ゆらぎ塩基対となるようにT(U)またはGにそれぞれ変換することが好適である。
3.成熟鎖が5位にGまたはT以外の塩基をもつ場合、スター鎖の相対する位置は、標準的なワトソン−クリック塩基対をなすように設計することが好適である。
4.成熟鎖12位とスター鎖の相対する位置との間には、ミスマッチが形成されることが好適である。ミスマッチ形成は、スター鎖の相対する位置が成熟鎖12位と同じ塩基をもつことで達成される。
5.成熟鎖の長さが18ヌクレオチド長またはそれ以上の場合、成熟鎖5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟18位およびスター鎖の相対する位置に同様に適用される。特に、成熟鎖18位がGまたはT(U)の場合、スター鎖の相対する位置は、ゆらぎ塩基対となるようにT(U)またはGにそれぞれ変換される。成熟鎖が18位にGまたはT(U)以外の塩基をもつ場合は、スター鎖の相対する位置は、標準的なワトソン−クリック塩基対を形成するように設計する。
6.成熟鎖の長さが19ヌクレオチド長またはそれ以上の場合、成熟鎖5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟19位およびスター鎖の相対する位置に、同様に適用される。特に、成熟鎖19位がGまたはT(U)の場合、スター鎖の相対する位置は、ゆらぎ塩基対となるようにT(U)またはGにそれぞれ変換される。成熟鎖が19位にGまたはT(U)以外の塩基をもつ場合は、スター鎖は、標準的なワトソン−クリック塩基対を形成するように設計する。
7.成熟鎖の長さが21ヌクレオチド長またはそれ以上の場合、成熟鎖5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟21位およびスター鎖の相対する位置に、同様に適用される。特に、成熟鎖21位がGまたはT(U)の場合、スター鎖の相対する位置は、ゆらぎ塩基対となるようにT(U)またはGにそれぞれ変換される。成熟鎖が21位にGまたはT(U)以外の塩基をもつ場合は、スター鎖は、標準的なワトソン−クリック塩基対を形成するように設計する。
本発明のshMIMIC類は、異なる成熟鎖の発現および活性レベルを標準化するのにとくに有用である。もし複数のshMIMIC類が全て同じスキャホールド配列を共有し、成熟鎖(およびスター鎖)配列だけが異なる場合、各shMIMICはDicerおよびRISCによって同程度に発現および処理されると考えられる。従って、細胞内で異なる内在性成熟鎖を発現する効果を、並べて比較することができる。もし各成熟鎖に相当する内在性pri−miRNA類を細胞内で発現した場合、各pri−miRNAはDicerおよびRISCによって程度が異なって処理されるので、このような比較は困難であろう。さらに、スター鎖は、内在性pri−miRNAそれぞれに対して機能性レベルを変化させる。もし内在性スキャホールド内にある成熟鎖の機能を観察する場合、スター鎖から成熟鎖への影響を見ることは不可能である。非内在性スキャホールド(例えば、shMIMIC)からmiRNAを発現する場合、前記スキャホールドの2次構造を維持するために、スター鎖を修飾するが、それにより、スター鎖配列は内在性スター鎖配列と同じではなくなる。従って、観察される機能は成熟鎖に関するものだけであり、shMIMICのスター鎖の機能は含まれない。
<成熟鎖を合理的に選択する実施形態>
また、別の一連の実施形態では、本発明のmiRNAスキャホールド類に挿入する成熟鎖配列類を合理的に設計する。miRNAの設計は、標的とする遺伝子内にある好ましい標的サイトを同定すること、および発現した分子内で構造要素が保持されるように選択した配列の周囲にあるスキャホールドを最適化することの2工程よりなる。標的サイトの同定は、いくつかの方法で行うことができる。一実施形態によれば、本発明は、1)スキャホールド中に埋め込んだ標的配列の機能にとって重要な特徴、および/または2)その機能にとって有害である特徴、を同定する方法を提供する。この方法は、(a)遺伝子を標的にするランダムに選択した配列セット(例えば、標的RNAに少なくとも部分的に相補的である成熟鎖配列類)を選択し、(b)これらの配列類を選択したスキャホールド内に組み込み、(c)スキャホールド内にある各配列の相対機能を測定し、(d)少なくとも1つの変換が機能に及ぼす影響があるかないかを測定し、および(e)工程(d)で得られた情報を用いて機能性配列類を選択するアルゴリズムを開発する、工程よりなる。
また、別の一連の実施形態では、本発明のmiRNAスキャホールド類に挿入する成熟鎖配列類を合理的に設計する。miRNAの設計は、標的とする遺伝子内にある好ましい標的サイトを同定すること、および発現した分子内で構造要素が保持されるように選択した配列の周囲にあるスキャホールドを最適化することの2工程よりなる。標的サイトの同定は、いくつかの方法で行うことができる。一実施形態によれば、本発明は、1)スキャホールド中に埋め込んだ標的配列の機能にとって重要な特徴、および/または2)その機能にとって有害である特徴、を同定する方法を提供する。この方法は、(a)遺伝子を標的にするランダムに選択した配列セット(例えば、標的RNAに少なくとも部分的に相補的である成熟鎖配列類)を選択し、(b)これらの配列類を選択したスキャホールド内に組み込み、(c)スキャホールド内にある各配列の相対機能を測定し、(d)少なくとも1つの変換が機能に及ぼす影響があるかないかを測定し、および(e)工程(d)で得られた情報を用いて機能性配列類を選択するアルゴリズムを開発する、工程よりなる。
配列類によって標的ノックダウン(工程(c))の効率を測定する方法には、標的遺伝子mRNAおよび/またはタンパクレベルを定量する方法が含まれる。mRNAについては、PCR法、ノーザンブロット法、および分岐DNA法を含む標準的技術が適用できる。タンパク質の定量には、ELISA法、ウエスタンブロット法などの方法が配列類の機能評価に使用できる。好ましいタンパク質検出方法としては、各配列の機能測定に使用できる各標的配列用の短い標的配列類を含む、2重ルシフェラーゼリポーターベクターシステム(例えば、psiCheck、Promega)などのリポーターシステムがある。
機能性および非機能性配列類を並べて分析することにより、特定のヌクレオチド類、熱力学的性質、2次構造などが機能を促進する、または機能に否定的に影響を及ぼす位置または領域を同定できる。こうしたプラスおよびマイナス要素を重み付けして合わせることで、選択アルゴリズムを構築することができる。
一実施例では、本発明はmiR−196a−2スキャホールドに対する機能性標的サイトを同定する方法を提供する。この方法には、約18−23個の塩基対(これより長いまたは短い配列類も具体的に考慮されるが)を有する潜在的配列類に対して選択基準(機能性および非機能性配列類をバイオインフォマティック分析することで決定される)を適用することが含まれる。ここで、選択基準は標的特有の基準ではなく独立したものである。好適な選択基準には、1)特定の位置にあるヌクレオチド類、2)特定の位置における位置特異的な熱力学的特性、3)標的配列内の可能な2次構造を削除または組み込むこと、およびその他の要因に関連してプラスおよびマイナスに重み付けした要素が含まれる。こうした選択基準を1つ以上適用することにより、miR−196a−2スキャホールドに挿入する配列類を合理的に設計することが可能になる。
また、ある実施形態では、前記選択基準は式によって具体化される。例えば、高機能をもつ非天然存在型miR−196a−2遺伝子標的配列類の成熟鎖(19ヌクレオチド長から、例えば、25ヌクレオチド長の成熟鎖でよい)の1−19番目までのヌクレオチドを決めるために、以下に示した式1を使用してよい。
式1:標的配列の逆相補鎖の1−19番目までのヌクレオチドを表わす。
スコア = (-500)*Al+(43.8)*Tl+(-21.3)*Cl+(-500)*Gl+(21.3)*T5+(18.8)*A6+(- 3)*T6+(25)*A7+(-41.3)*G7+(21.3)*T8+(-16.3)*C8+(37.5)*T12+(-18.8)*G12+(27.5)*T13+(-22.5)*C13+(21.3)*T15+(-17.5)*G15+(-18.8)*G16+(-18.8)*G17+(16.3)*T18+(- 17.5)*G18+(21.3)*T19+(28.8)*C19+(-35)*G19
(式1)
ここで、「A」はアデニンを表し、「G」はグアニンを表し、「T」はチミンを表し、および「C」はチトシンを表す。さたに、各塩基記号に付いている番号は(例えば、A1)、標的配列の逆相補鎖におけるその塩基の位置を表す。このように、このアルゴリズムにおける逆相補鎖(RC)ヌクレオチド1は、標的RNA内のヌクレオチド19と相補的になる(図2参照)。また、miRNAスキャホールドに挿入した成熟鎖ヌクレオチド1に対し、ヌクレオチド19は標的mRNA塩基対またはゆらぎ塩基対を形成する。以下の表1に、整列させたヌクレオチド類の位置を示す。ここで、M1−M19は成熟鎖のヌクレオチド1−ヌクレオチド19であり、R1−R19は標的RNAのヌクレオチド1−ヌクレオチド19であり、ヌクレオチドS1−S19はスター鎖のヌクレオチド1−ヌクレオチド19である。
(式1)
ここで、「A」はアデニンを表し、「G」はグアニンを表し、「T」はチミンを表し、および「C」はチトシンを表す。さたに、各塩基記号に付いている番号は(例えば、A1)、標的配列の逆相補鎖におけるその塩基の位置を表す。このように、このアルゴリズムにおける逆相補鎖(RC)ヌクレオチド1は、標的RNA内のヌクレオチド19と相補的になる(図2参照)。また、miRNAスキャホールドに挿入した成熟鎖ヌクレオチド1に対し、ヌクレオチド19は標的mRNA塩基対またはゆらぎ塩基対を形成する。以下の表1に、整列させたヌクレオチド類の位置を示す。ここで、M1−M19は成熟鎖のヌクレオチド1−ヌクレオチド19であり、R1−R19は標的RNAのヌクレオチド1−ヌクレオチド19であり、ヌクレオチドS1−S19はスター鎖のヌクレオチド1−ヌクレオチド19である。
機能性および非機能性配列類を詳細に検討することにより、非天然存在型miR−196a−2miRNA類の成熟鎖1位にはUが好適であると同定した。従って、成熟鎖1位におけるUは非常に好適である。このことを考慮すると、標的の逆相補鎖の1位の「A」または「G」は、かなりマイナスに重み付けされる(−500)。たとえ重み付けの程度が比較的小さくても、1位に「C」もまた選択される。その理由は、1位の[C]によって、成熟−標的2本鎖中にGUゆらぎ塩基対が形成されるようにできるからである。一方、標的のRC1位における「T」は非常に好適である(+43.8)。ここで、「U」はRNA分子内にあるヌクレオチドを意味し、「T」はRNA分子のcDNA内にあるヌクレオチドを意味する。
ここで、miR−196a−2に対して、21ヌクレオチド内在性成熟鎖配列(3’末端がGGである)および22ヌクレオチド内在性成熟鎖配列(3’末端がGGGである)をともに支持する証拠がある。もし、非天然存在型miR−196a−2の成熟鎖が、3’端にヌクレオチド類を追加して19ヌクレオチド長よりも長い場合、スター鎖もまた、スター鎖および成熟鎖が同じ長さになるように、5’端に追加ヌクレオチドを有する。例えば、もし成熟鎖が21ヌクレオチド長である場合、スター鎖もまた上記配列にS15位の2塩基類を追加すると、21ヌクレオチド長になる。式1のアルゴリズムを用いる実施形態および、成熟鎖が21ヌクレオチド配列である実施形態では、成熟鎖(成熟鎖のヌクレオチド1はUが好適である)の塩基2ないし塩基19の塩基類は、式1のアルゴリズムによって決定され、塩基20と塩基21は、内在性miR−196a−2成熟鎖配列をミミックするようにGであってよいが、必ずしもGでなくてもよい。もし、成熟鎖の塩基20と塩基21がGGである場合、スター鎖の相対する位置にある塩基を、内在性成熟鎖−スター鎖2本鎖内と同じくCC、UU、UCに、またはワトソン−クリックまたはゆらぎ塩基対を形成するCUにすることができる。あるいは、20位及び21位をGGにして、スター鎖内の相対する位置にあるヌクレオチドにミスマッチ(例えば、G−GミスマッチまたはG−Aミスマッチ)させることができる。あるいは、20位及び21位を、標的RNAと塩基対を形成する配列類で構成することができる。この場合、相対するスター鎖にあるヌクレオチド類は、ワトソン−クリック塩基対、ゆらぎ塩基対、またはミスマッチを形成することが可能である。
上で述べたように、miR−196a−2に対して、21ヌクレオチド内在性成熟鎖および22ヌクレオチド内在性成熟鎖がともに存在することを支持する証拠がある。従って、同様に成熟鎖が22ヌクレオチド長である場合、スター鎖も上記配列においてS1の5’位に3つの塩基類を追加すると22ヌクレオチド長となる。式1のアルゴリズムを用い、成熟鎖が22ヌクレオチド配列である実施形態の場合、成熟鎖の塩基2ないし塩基19の塩基類は式1のアルゴリズムによって決定される。20、21および22番目の塩基類は、好適にはヌクレオチド1がUである内在性miR−196a−2成熟鎖をミミックするためにGであってもよいが、必ずGである必要はない。前記成熟鎖の20−22番目の塩基類がGGGである場合、スター鎖の相対する位置にある塩基類はワトソン−クリック塩基対またはゆらぎ塩基対を形成することができる。例えば、前記成熟鎖の20−22番目の塩基類がGGGである場合、この配列に相対するスター鎖配列は、この位置で内在性成熟鎖―スター鎖2本鎖をミミックするCUCでよい。または、20、21、および22位にはGGGが可能であり、これらのヌクレオチド類はスター鎖中、相対する位置にあるヌクレオチド類と、例えば、G−GミスマッチまたはG−Aミスマッチのように、ミスマッチすることが可能である。あるいは、20−22位は、標的RNAと塩基対を形成する配列類からなることが可能である。この場合、相対するスター鎖上にあるヌクレオチド類は、ワトソン−クリック塩基対、ゆらぎ塩基対、またはミスマッチを形成することができる。
式1は、標的ヌクレオチドの位置傾向をもつ逆相補配列を示す。このように、式1は、例えば、(1)標的RNAの逆相補配列を決定し、(2)この配列にアルゴリズムを適用して所望のスコア(例えば、最も高いスコア、または最も高い複数のスコアのうちの1スコア)をもつ19ヌクレオチド部分配列を決定することに用いられる。こうして決定した配列類は、続いて、非天然存在型miRNA−196a−2類を生成するためにmiRNA−196a−2スキャホールド内に導入される。
式1は、各条件が標的配列のRCの塩基についてランク順を示すように、一連の条件によって表すことも可能である。
条件1:標的配列のRCの1位には、CよりTが好ましく、GおよびAは各々好ましくない。
条件2:標的配列のRCの5位には、G、CおよびAの各々よりTが好ましい。
条件3:標的配列のRCの6位には、GおよびCの各々よりAが好ましく、さらに、TよりGおよびCの各々が好ましい。
条件4:標的配列のRCの7位には、CおよびTの各々よりAが好ましく、さらに、GよりCおよびTの各々が好ましい。
条件5:標的配列のRCの8位には、AおよびGの各々よりTが好ましく、さらに、CよりAおよびGの各々が好ましい。
条件6:標的配列のRCの12位には、AおよびCの各々よりTが好ましく、さらに、GよりAおよびCの各々が好ましい。
条件7:標的配列のRCの13位には、AおよびGの各々よりTが好ましく、さらに、CよりAおよびGの各々が好ましい。
条件8:標的配列のRCの15位には、AおよびCの各々よりTが好ましく、さらに、GよりAおよびCの各々が好ましい。
条件9:標的配列のRCの16位には、GよりA、C、およびTの各々が好ましい。
条件10:標的配列のRCの17位には、GよりA、C、およびTの各々が好ましい。
条件11:標的配列のRCの18位には、AおよびCの各々よりTが好ましく、さらに、GよりAおよびCの各々が好ましい。
条件12:標的配列のRCの19位には、TよりCが好ましく、AよりTが好ましく、さらに、GよりAが好ましい。
条件1:標的配列のRCの1位には、CよりTが好ましく、GおよびAは各々好ましくない。
条件2:標的配列のRCの5位には、G、CおよびAの各々よりTが好ましい。
条件3:標的配列のRCの6位には、GおよびCの各々よりAが好ましく、さらに、TよりGおよびCの各々が好ましい。
条件4:標的配列のRCの7位には、CおよびTの各々よりAが好ましく、さらに、GよりCおよびTの各々が好ましい。
条件5:標的配列のRCの8位には、AおよびGの各々よりTが好ましく、さらに、CよりAおよびGの各々が好ましい。
条件6:標的配列のRCの12位には、AおよびCの各々よりTが好ましく、さらに、GよりAおよびCの各々が好ましい。
条件7:標的配列のRCの13位には、AおよびGの各々よりTが好ましく、さらに、CよりAおよびGの各々が好ましい。
条件8:標的配列のRCの15位には、AおよびCの各々よりTが好ましく、さらに、GよりAおよびCの各々が好ましい。
条件9:標的配列のRCの16位には、GよりA、C、およびTの各々が好ましい。
条件10:標的配列のRCの17位には、GよりA、C、およびTの各々が好ましい。
条件11:標的配列のRCの18位には、AおよびCの各々よりTが好ましく、さらに、GよりAおよびCの各々が好ましい。
条件12:標的配列のRCの19位には、TよりCが好ましく、AよりTが好ましく、さらに、GよりAが好ましい。
また、ある実施形態では、前記条件の1以上の条件または全ての条件が、成熟鎖配列類を決定するために適用される。例えば、前記条件は、(1)標的RNAの逆相補配列を決定し、(2)19ヌクレオチド部分配列(類)を決定するために前記条件から1つ以上の条件を適用することに用いられる。こうして決定した配列類は、続いて、非天然存在型miRNA−196a−2 miRNA類を生成するためにmiRNA−196a−2 miRNAスキャホールド内に導入される。好適な実施形態としては、成熟鎖1位はT/Uである。
また、標的RNAヌクレオチドの傾向(表1のR1−R19参照)を直接示すように、式1を同じ意味で表すことも可能であることを、当業者は理解しよう。 このことは、式1の各ヌクレオチドの傾向を標的RNA(表1参照)の相対する相補ヌクレオチドで置き換えることによって、実施される。所望の標的RNA配列が決まり次第、その逆相補配列(好適には、1位がT/U)を、成熟鎖を形成するmiRNA−196a−2 miRNAスキャホールド内に導入する。従って、元々の式1が、M2が「G」であることを示したとすれば、それを発展させた式ではR18が「C」であることを示す。
同様にして、式1が標的サイトを記述するために用いられる場合、各条件が標的RNAの塩基(例えば、表のR1−R19塩基類参照)についてランク順位を表すように、一連の条件として示すことも可能である。
条件1:R1では、AよりGが好ましく、UよりAが好ましく、CよりUが好ましい。
条件2:R2では、UおよびGの各々よりAが好ましく、CよりUおよびGの各々が好ましい。
条件3:R3にでは、CよりU、GおよびAの各々が好ましい。
条件4:R4では、CよりU、GおよびAの各々が好ましい。
条件5:R5では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件6:R7では、UおよびCの各々よりAが好ましく、さらに、GよりUおよびCの各々が好ましい。
条件7:R8では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件8:R12はで、UおよびCの各々よりAが好ましく、さらに、GよりUおよびCの各々が好ましい。
条件9:R13では、GおよびAの各々よりUが好ましく、さらに、CよりGおよびAの各々が好ましい。
条件10:R14では、CおよびGの各々よりUが好ましく、さらに、AよりCおよびGの各々が好ましい。
条件11:R15では、C、GおよびUの各々よりAが好ましい。
条件12:R19では、GよりAが好ましく、CおよびUの各は好ましくない。
条件1:R1では、AよりGが好ましく、UよりAが好ましく、CよりUが好ましい。
条件2:R2では、UおよびGの各々よりAが好ましく、CよりUおよびGの各々が好ましい。
条件3:R3にでは、CよりU、GおよびAの各々が好ましい。
条件4:R4では、CよりU、GおよびAの各々が好ましい。
条件5:R5では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件6:R7では、UおよびCの各々よりAが好ましく、さらに、GよりUおよびCの各々が好ましい。
条件7:R8では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件8:R12はで、UおよびCの各々よりAが好ましく、さらに、GよりUおよびCの各々が好ましい。
条件9:R13では、GおよびAの各々よりUが好ましく、さらに、CよりGおよびAの各々が好ましい。
条件10:R14では、CおよびGの各々よりUが好ましく、さらに、AよりCおよびGの各々が好ましい。
条件11:R15では、C、GおよびUの各々よりAが好ましい。
条件12:R19では、GよりAが好ましく、CおよびUの各は好ましくない。
前記条件の1つ以上の条件または全ての条件が、所望の標的RNA配列を決定するために適用してよい。例えば、前記条件の1つ以上の条件は、19ヌクレオチド部分配列(類)を決定するために所望の標的RNA配列に適用される。こうして決定した部分配列(好適には1位にTを有する)の逆相補配列は、続いて、非天然存在型miRNA−196a−2 miRNAを生成するために、成熟鎖としてmiRNA−196a−2 miRNAスキャホールド内に導入される。好適な実施形態としては、R19がAとなるように条件12が選ばれる。
また、別の実施形態では、本発明は、高機能性非天然存在型miRNA−196a−2 miRNAの成熟鎖(21−25ヌクレオチド成熟鎖であってよい)の1−21番目の塩基類(5’から3’方向に付番される)を決定するために別のアルゴリズムを提供する。下記の式2参照。
式2: 標的配列の逆相補配列の1−21ヌクレオチド類に関する。
式2: 標的配列の逆相補配列の1−21ヌクレオチド類に関する。
スコア=
(-500)*Al+(43.75)*Tl+(-21.25)*Cl+(-500)*Gl+(-36.7)*C3+(-33.3)*A5+(50)*T5+(- 46.7)*C5+(37.5)*A6+(25)*A7+(29.2)*T7+(-41.25)*G7+(21.25)*T8+(-16.25)*C8+(45.8)*T12+(-18.75)*G12+(58.3)*T13+(-37.5)*C13+(-36.7)*C14+(21.25)*T15+(-17.5)*G15+(-36.7)*C16+(-18.75)*G16+(40)*T17+(-18.75)*G17+(16.25)*T18+(-17.5)*G18+(- 33.3)*A19+(21.25)*T19+(28.75)*C19+(-35)*G19+(-23.3)*C20+(50) *T21
(式2)
ここで、「A」はアデニンを表し、「G」はグアニンを表し、「T」はチミンを表し、「C」はシトシンを表す。また、各塩基の記号に付く数字は(例えば、A1)標的mRNAの逆相補配列中の塩基の位置を表す。このように、前記アルゴリズムによる逆相補ヌクレオチド1は、標的mRNAのヌクレオチド21の相補配列である(図2参照)。下記の表2に、配列したヌクレオチドの位置を示す。ここで、M1−M21は、成熟鎖の1−21番目のヌクレオチド類であり、R1−R21は標的RNAの1−21番目のヌクレオチド類であり、ヌクレオチド類S1−S21はスター鎖の1−21番目のヌクレオチド類である。
(-500)*Al+(43.75)*Tl+(-21.25)*Cl+(-500)*Gl+(-36.7)*C3+(-33.3)*A5+(50)*T5+(- 46.7)*C5+(37.5)*A6+(25)*A7+(29.2)*T7+(-41.25)*G7+(21.25)*T8+(-16.25)*C8+(45.8)*T12+(-18.75)*G12+(58.3)*T13+(-37.5)*C13+(-36.7)*C14+(21.25)*T15+(-17.5)*G15+(-36.7)*C16+(-18.75)*G16+(40)*T17+(-18.75)*G17+(16.25)*T18+(-17.5)*G18+(- 33.3)*A19+(21.25)*T19+(28.75)*C19+(-35)*G19+(-23.3)*C20+(50) *T21
(式2)
ここで、「A」はアデニンを表し、「G」はグアニンを表し、「T」はチミンを表し、「C」はシトシンを表す。また、各塩基の記号に付く数字は(例えば、A1)標的mRNAの逆相補配列中の塩基の位置を表す。このように、前記アルゴリズムによる逆相補ヌクレオチド1は、標的mRNAのヌクレオチド21の相補配列である(図2参照)。下記の表2に、配列したヌクレオチドの位置を示す。ここで、M1−M21は、成熟鎖の1−21番目のヌクレオチド類であり、R1−R21は標的RNAの1−21番目のヌクレオチド類であり、ヌクレオチド類S1−S21はスター鎖の1−21番目のヌクレオチド類である。
また、成熟鎖が21ヌクレオチド長よりも長い場合(例えば、22または23ヌクレオチド長)、スター鎖もまた、スター鎖および成熟鎖が同じ長さになるように、5’端に追加ヌクレオチドを有する。例えば、成熟鎖が22ヌクレオチド長(内在性miR−196a−2成熟鎖の長さである)である場合、スター鎖もまた上記配列にS15位の追加2塩基を加えて、22ヌクレオチド長になる。式2のアルゴリズムが用いられる実施形態および、成熟鎖が22ヌクレオチド配列である実施形態では、成熟鎖(成熟鎖のヌクレオチド1はUが好適である)の2−21番目の塩基類は、式2のアルゴリズムによって決定され、22番目の塩基は、miR−196a−2の内在性22ヌクレオチド成熟鎖中の同じヌクレオチドである、例えば、Gであってよい。もし、成熟鎖の22番目の塩基がGである場合、スター鎖の相対する位置にある塩基を、内在性miR−196a−2にある塩基と同じCに、または、ワトソン−クリック塩基対またはゆらぎ塩基対を形成するようにUとすることができる。あるいは、22位をGにして、スター鎖内の相対する位置にあるヌクレオチドにミスマッチ(例えば、G−GミスマッチまたはG−Aミスマッチ)させることができる。あるいは、22位を、標的RNAと塩基対を形成するヌクレオチドにすることができる。この場合、相対するスター鎖にあるヌクレオチドは、ワトソン−クリック塩基対、ゆらぎ塩基対、またはミスマッチを形成することが可能である。
式1と同様に、式2は、標的配列ヌクレオチドの位置傾向を有する逆相補配列を示す。このように、式2は、例えば、(1)標的RNAの逆相補配列を決定し、(2)この配列にアルゴリズムを適用して所望のスコア(例えば、最も高いスコア、または最も高い複数のスコアのうちの1スコア)をもつ21ヌクレオチド部分配列を決定することに用いられる。こうして決定した配列類は、続いて、非天然存在型miRNA−196a−2類を生成するためにmiRNA−196a−2スキャホールド内に導入される。
各条件が標的配列の逆相補配列の塩基についてランク順を示すように、式2を一連の条件によって表すことも可能である。
条件1:標的配列の逆相補配列1位は、T>Cであり、AおよびGの各は好ましくない。
条件2:標的配列の逆相補配列3位は、A、T、G>C。
条件3:標的配列の逆相補配列5位は、T>G>A>C。
条件4:標的配列の逆相補配列6位は、A>G、C、T。
条件5:標的配列の逆相補配列7位は、T>A>C>G。
条件6:標的配列の逆相補配列8位は、T>A、G>C。
条件7:標的配列の逆相補配列12位は、T>A、C>G。
条件8:標的配列の逆相補配列13位は、T>A、G>C。
条件9:標的配列の逆相補配列14位は、A、G、T>C。
条件10:標的配列の逆相補配列15位は、T>A、C>G。
条件11:標的配列の逆相補配列16位は、A、T>G>C。
条件12:標的配列の逆相補配列17位は、T>A、C>G。
条件13:標的配列の逆相補配列18位は、T>A、C>G。
条件14:標的配列の逆相補配列19位は、C>T>A>G。
条件15:標的配列の逆相補配列20位は、A、G、T>C。
条件16:標的配列の逆相補配列21位は、T>A、G、C。
ここで、>は他の塩基よりある塩基が好ましいことを示す。例えば、W>X、Y>ZはXおよびYの各よりWが好ましく、ZよりXおよびYの各々が好ましいことを示す。ある実施形態では、前記条件の1つ以上の条件または全ての条件が、成熟鎖配列類を決定するために適用される。例えば、前記条件は、(1)標的RNAの逆相補配列を決定し、(2)21ヌクレオチド部分配列(類)を決定するために前記条件から1つ以上の条件を適用することに用いられる。こうして決定した配列類は、続いて、非天然存在型miRNA−196a−2 miRNA類を生成するためにmiRNA−196a−2 miRNAスキャホールド内に導入される。好適な実施形態としては、成熟鎖1位は「T」である。
条件1:標的配列の逆相補配列1位は、T>Cであり、AおよびGの各は好ましくない。
条件2:標的配列の逆相補配列3位は、A、T、G>C。
条件3:標的配列の逆相補配列5位は、T>G>A>C。
条件4:標的配列の逆相補配列6位は、A>G、C、T。
条件5:標的配列の逆相補配列7位は、T>A>C>G。
条件6:標的配列の逆相補配列8位は、T>A、G>C。
条件7:標的配列の逆相補配列12位は、T>A、C>G。
条件8:標的配列の逆相補配列13位は、T>A、G>C。
条件9:標的配列の逆相補配列14位は、A、G、T>C。
条件10:標的配列の逆相補配列15位は、T>A、C>G。
条件11:標的配列の逆相補配列16位は、A、T>G>C。
条件12:標的配列の逆相補配列17位は、T>A、C>G。
条件13:標的配列の逆相補配列18位は、T>A、C>G。
条件14:標的配列の逆相補配列19位は、C>T>A>G。
条件15:標的配列の逆相補配列20位は、A、G、T>C。
条件16:標的配列の逆相補配列21位は、T>A、G、C。
ここで、>は他の塩基よりある塩基が好ましいことを示す。例えば、W>X、Y>ZはXおよびYの各よりWが好ましく、ZよりXおよびYの各々が好ましいことを示す。ある実施形態では、前記条件の1つ以上の条件または全ての条件が、成熟鎖配列類を決定するために適用される。例えば、前記条件は、(1)標的RNAの逆相補配列を決定し、(2)21ヌクレオチド部分配列(類)を決定するために前記条件から1つ以上の条件を適用することに用いられる。こうして決定した配列類は、続いて、非天然存在型miRNA−196a−2 miRNA類を生成するためにmiRNA−196a−2 miRNAスキャホールド内に導入される。好適な実施形態としては、成熟鎖1位は「T」である。
また、式1と同様に、標的RNAヌクレオチドの傾向(表2のR1−R21参照)を直接示すように、式1を同じ意味で表すことも可能である。 このことは、式2の各ヌクレオチドの傾向を標的RNA(表2参照)の相対する相補ヌクレオチドで置き換えることによって、実施される。
同様にして、各条件が標的RNAの塩基(例えば、表2のR1−R21塩基類参照)についてランク順位を表すように、式2を一連の条件として示すことも可能である。
条件1:R1では、U、C、およびGの各よりAが好ましい。
条件2:R2では、GよりCよりU、CおよびAの各々が好ましい。
条件3:R3にでは、AよりCが好ましく、UよりAが好ましく、CよりUが好ましい。
条件4:R4では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件5:R5では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件6:R6では、CよりUおよびAの各々が好ましく、さらに、GよりCが好ましい。
条件7:R7では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件8:R8では、GよりU、CおよびAの各々が好ましい。
条件9:R9では、UおよびCの各々よりAが好ましく、さらに、GよりUおよびCの各々が好ましい。
条件10:R10では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件11:R14では、UおよびCの各々よりAが好ましく、さらに、GよりUおよびCの各々が好ましい。
条件12:R15では、UよりAが好ましく、GよりUが好ましく、CよりGが好ましい。
条件13:R16では、C、G、およびAの各々よりUが好ましい。
条件14:R17では、CよりAが好ましく、UよりCが好ましく、GよりUが好ましい。
条件15:R19では、GよりU、AおよびCの各々が好ましい。
条件16:R21では、GよりAが好ましく、UおよびCの各々は好ましくない。
条件1:R1では、U、C、およびGの各よりAが好ましい。
条件2:R2では、GよりCよりU、CおよびAの各々が好ましい。
条件3:R3にでは、AよりCが好ましく、UよりAが好ましく、CよりUが好ましい。
条件4:R4では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件5:R5では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件6:R6では、CよりUおよびAの各々が好ましく、さらに、GよりCが好ましい。
条件7:R7では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件8:R8では、GよりU、CおよびAの各々が好ましい。
条件9:R9では、UおよびCの各々よりAが好ましく、さらに、GよりUおよびCの各々が好ましい。
条件10:R10では、UおよびGの各々よりAが好ましく、さらに、CよりUおよびGの各々が好ましい。
条件11:R14では、UおよびCの各々よりAが好ましく、さらに、GよりUおよびCの各々が好ましい。
条件12:R15では、UよりAが好ましく、GよりUが好ましく、CよりGが好ましい。
条件13:R16では、C、G、およびAの各々よりUが好ましい。
条件14:R17では、CよりAが好ましく、UよりCが好ましく、GよりUが好ましい。
条件15:R19では、GよりU、AおよびCの各々が好ましい。
条件16:R21では、GよりAが好ましく、UおよびCの各々は好ましくない。
前記条件の1つ以上の条件または全ての条件を、所望の標的RNA配列を決定するために適用してよい。例えば、前記条件の1つ以上の条件を、ヌクレオチド部分配列(類)を決定するために所望の標的RNA配列に適用することにより、前記条件は用いられる。こうして決定した部分配列(好適には1位にT/Uを有する)の逆相補配列は、続いて、非天然存在型miRNA−196a−2 miRNAを生成するために、成熟鎖としてmiRNA−196a−2 miRNAスキャホールド内に導入される。好適な実施形態としては、成熟鎖の1位は「T/U」である。
位置特異的要因、特に、全体のGC含有量、シード領域内のGC含有量、およびテトラヌクレオチドの存在に焦点をあてた追加の重み付け要素類を、式1、式2、またはその誘導体の機能性をさらに促進するために加えることも可能である。例えば、成熟鎖中の以下に述べるどの要素もそれら要素類に含まれる。
a.−3*(#GC)
b.少なくとも「AAAA」が1個ある場合は−100
c.少なくとも「TTTT」が1個ある場合は−100
d.少なくとも「GGGG」が1個ある場合は−100
e.少なくとも「CCCC」が1個ある場合は−100
f.2−8位中>GCの場合は−100
g.>10GCの場合は−100
ここで、「#GCの#」は標的の逆相補配列中の(または、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中の)GおよびCヌクレオチド類の数を表す。
「AAAA」は標的の逆相補配列中の全てのAを含有するテトラヌクレオチドを表す。ここで、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中の「UUUU」と同じ意味を表す。「
TTTT」は標的の逆相補配列中の全てのTを含有するテトラヌクレオチドを表す。ここで、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中の「AAAA」と同じ意味を表す。
「GGGG」は標的の逆相補配列中の全てのTを含有するテトラヌクレオチドを表す。ここで、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中の「CCCC」と同じ意味を表す。「CCCC」は標的の逆相補配列中の全てのTを含有するテトラヌクレオチドを表す。ここで、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中の「GGGG」と同じ意味を表す。
「2−8位中>4GC」は、成熟鎖(例えば、シード領域))の2位―8位にある5個以上のGおよび/またはCヌクレオチドを表す。ここで、式2が標的RNAの傾向として表わされる場合にはR14−R20位にある、または、式1が標的RNAの傾向として表わされる場合にはR12−R18位にある、5個以上のGおよび/またはCヌクレオチドと同じ意味を表す。
「>10GC」は、標的配列の逆相補配列中にある11個以上のGおよび/またはCヌクレオチドを表す。ここで、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中にある11個以上のGおよび/またはCヌクレオチドと同じ意味を表す。
a.−3*(#GC)
b.少なくとも「AAAA」が1個ある場合は−100
c.少なくとも「TTTT」が1個ある場合は−100
d.少なくとも「GGGG」が1個ある場合は−100
e.少なくとも「CCCC」が1個ある場合は−100
f.2−8位中>GCの場合は−100
g.>10GCの場合は−100
ここで、「#GCの#」は標的の逆相補配列中の(または、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中の)GおよびCヌクレオチド類の数を表す。
「AAAA」は標的の逆相補配列中の全てのAを含有するテトラヌクレオチドを表す。ここで、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中の「UUUU」と同じ意味を表す。「
TTTT」は標的の逆相補配列中の全てのTを含有するテトラヌクレオチドを表す。ここで、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中の「AAAA」と同じ意味を表す。
「GGGG」は標的の逆相補配列中の全てのTを含有するテトラヌクレオチドを表す。ここで、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中の「CCCC」と同じ意味を表す。「CCCC」は標的の逆相補配列中の全てのTを含有するテトラヌクレオチドを表す。ここで、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中の「GGGG」と同じ意味を表す。
「2−8位中>4GC」は、成熟鎖(例えば、シード領域))の2位―8位にある5個以上のGおよび/またはCヌクレオチドを表す。ここで、式2が標的RNAの傾向として表わされる場合にはR14−R20位にある、または、式1が標的RNAの傾向として表わされる場合にはR12−R18位にある、5個以上のGおよび/またはCヌクレオチドと同じ意味を表す。
「>10GC」は、標的配列の逆相補配列中にある11個以上のGおよび/またはCヌクレオチドを表す。ここで、式1または式2が標的RNAの傾向として表わされる場合には標的RNA中にある11個以上のGおよび/またはCヌクレオチドと同じ意味を表す。
同様にして、式1および式2が上で述べたように一連の条件として表わされる場合、追加される重み付け要素を別の追加条件として表わしてもよい。例えば、式1および式2が一連の条件として表わされる場合、追加される重み付け要素を以下の条件として表わしてもよい。ここで、条件の1つ以上のまたは全ての条件は所望の配列類を選択するために用いてもよい。
A) 標的配列の逆相補配列は、AAAA、UUUU、GGGG、およびCCCC
からなる群より選ばれるテトラヌクレオチド配列を含まない。または、同じ意味で、標的RNA配列は、AAAA、UUUU、GGGG、またはCCCCを含まない。
B) 標的配列の逆相補配列は、全体で10個以下のG+C含有量をもつ。または、同じ意味で、標的RNA配列類は、全体で11個以上のG+C含有量をもたない。
C) 成熟鎖は、シード領域に4個以下のG+C含有量をもつ。または、同じ意味で、前記成熟鎖のシード領域に相対する標的RNA配列の塩基類は、4個以下のG+C含有量をもつ。
A) 標的配列の逆相補配列は、AAAA、UUUU、GGGG、およびCCCC
からなる群より選ばれるテトラヌクレオチド配列を含まない。または、同じ意味で、標的RNA配列は、AAAA、UUUU、GGGG、またはCCCCを含まない。
B) 標的配列の逆相補配列は、全体で10個以下のG+C含有量をもつ。または、同じ意味で、標的RNA配列類は、全体で11個以上のG+C含有量をもたない。
C) 成熟鎖は、シード領域に4個以下のG+C含有量をもつ。または、同じ意味で、前記成熟鎖のシード領域に相対する標的RNA配列の塩基類は、4個以下のG+C含有量をもつ。
ここで、成熟鎖を記載する場合、標的RNA配列を記載するためにヌクレオチドUを用いることが可能である。または、前記RNAのcDNAを記載するために、ヌクレオチドTを用いることが可能である。
また、(例えば、ヘアピン構造などの2次構造をもつことができる標的配列を除外することに焦点をあてた追加の重み付け要素を、選択アルゴリズムに加えることも可能である。
また、配列類を選択する方法はどれも、細胞ストレスをもつモチーフを含有する配列類を選択する工程をさらに有することができる。このようなモチーフとしては、例えば、毒性モチーフ(米国特許出願第2005/0203043号明細書(2005年9月15日)参照)が含まれる。上で述べたアルゴリズムは、標的の配列を入力すると自動的に最適化された標的配列を出力するコンピュータプログラムとともに使用してもよく、またはコンピュータプログラムを用いることなく使用してもよい。前記コンピュータプログラムは、例えば、局所端末またはパーソナルコンピュータから内部ネットワークまたはインターネットを通してアクセス可能である。
また、配列類を選択する方法はどれも、特定のシード領域(成熟鎖2−7位または2−8位)配列類をもつ標的配列類を選択する工程をさらに有することができる。限定的でない例としては、内在性に発現した1つ以上のマイクロRNA類のシード類の1つと完全一致するシード類をもつ標的配列類を除外することが可能である。また別の例では、中程度または高い頻度でシード相補配列が現れるシード類を除外することが可能である。米国特許出願第11/724,346号明細書(2007年3月15日出願)に、中程度または高い頻度でシード相補配列が現れるシード類の重要性が記載される。
最適な成熟鎖配列類が得られると、上で述べたように、これらの配列類はmiR−196a−2スキャホールド類に導入される。スター鎖は、そのほとんどが成熟鎖の逆相補配列であるが、内在性miR−196a−2の内在性成熟鎖−スター鎖の構造をミミックする局所構造をもつように変換部分をもつことが好ましい。例えば、スター鎖の特性は、図3に示し以下に詳しく記載する1つ以上の特性を有していてよい。
1.成熟鎖の1位がUである場合(上記のように、これは好適ではあるが必須条件ではない)、スター鎖の相対する位置は、常にゆらぎ塩基対が形成されるようにGが好ましい。
2.成熟鎖の5位がGまたはT(U)である場合、スター鎖の相対する位置は、ゆらぎ塩基対が形成されるように、それぞれT(U)またはGに変換されることが好ましい。
3.成熟鎖が5位にGまたはT以外の基をもつ場合、スター鎖の相対する位置は、標準的ワトソン−クリック塩基対が形成されるように設計される。
4.成熟鎖の12位とスター鎖の相対する位置との間に、ミスマッチが形成されることが好ましい。これは、スター鎖の相対する位置に、成熟鎖の12位と同じ塩基をもつようにすることで達成できる。
5.成熟鎖が18ヌクレオチド長またはそれよりも長い場合、成熟鎖の5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟鎖の18位およびスター鎖の相対する位置に対して同じように適用される。具体的には、成熟鎖の18位がGまたはT(U)である場合、ゆらぎ塩基対が形成されるように、スター鎖の相対する位置は、それぞれT(U)またはGに変換される。成熟鎖が18位にGまたはT以外の基をもつ場合、スター鎖のこの位置に相対する位置は、標準的ワトソン−クリック塩基対が形成されるように設計される。
6.成熟鎖が19ヌクレオチド長またはそれよりも長い場合、成熟鎖の5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟鎖の19位およびスター鎖の相対する位置に対して同じように適用される。具体的には、成熟鎖の19位がGまたはT(U)である場合、ゆらぎ塩基対が形成されるように、スター鎖の相対する位置は、それぞれT(U)またはGに変換される。成熟鎖が19位にGまたはT(U)以外の基をもつ場合、スター鎖は、標準的ワトソン−クリック塩基対が形成されるように設計される。
7.成熟鎖が21ヌクレオチド長またはそれよりも長い場合、成熟鎖の5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟鎖の21位およびスター鎖の相対する位置に対して同じように適用される。具体的には、成熟鎖の21位がGまたはT(U)である場合、ゆらぎ塩基対が形成されるように、スター鎖の相対する位置は、それぞれT(U)またはGに変換される。成熟鎖が21位にGまたはT(U)以外の基をもつ場合、スター鎖は、標準的ワトソン−クリック塩基対が形成されるように設計される。
1.成熟鎖の1位がUである場合(上記のように、これは好適ではあるが必須条件ではない)、スター鎖の相対する位置は、常にゆらぎ塩基対が形成されるようにGが好ましい。
2.成熟鎖の5位がGまたはT(U)である場合、スター鎖の相対する位置は、ゆらぎ塩基対が形成されるように、それぞれT(U)またはGに変換されることが好ましい。
3.成熟鎖が5位にGまたはT以外の基をもつ場合、スター鎖の相対する位置は、標準的ワトソン−クリック塩基対が形成されるように設計される。
4.成熟鎖の12位とスター鎖の相対する位置との間に、ミスマッチが形成されることが好ましい。これは、スター鎖の相対する位置に、成熟鎖の12位と同じ塩基をもつようにすることで達成できる。
5.成熟鎖が18ヌクレオチド長またはそれよりも長い場合、成熟鎖の5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟鎖の18位およびスター鎖の相対する位置に対して同じように適用される。具体的には、成熟鎖の18位がGまたはT(U)である場合、ゆらぎ塩基対が形成されるように、スター鎖の相対する位置は、それぞれT(U)またはGに変換される。成熟鎖が18位にGまたはT以外の基をもつ場合、スター鎖のこの位置に相対する位置は、標準的ワトソン−クリック塩基対が形成されるように設計される。
6.成熟鎖が19ヌクレオチド長またはそれよりも長い場合、成熟鎖の5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟鎖の19位およびスター鎖の相対する位置に対して同じように適用される。具体的には、成熟鎖の19位がGまたはT(U)である場合、ゆらぎ塩基対が形成されるように、スター鎖の相対する位置は、それぞれT(U)またはGに変換される。成熟鎖が19位にGまたはT(U)以外の基をもつ場合、スター鎖は、標準的ワトソン−クリック塩基対が形成されるように設計される。
7.成熟鎖が21ヌクレオチド長またはそれよりも長い場合、成熟鎖の5位およびスター鎖の相対する位置に適用される条件と同じ条件が、成熟鎖の21位およびスター鎖の相対する位置に対して同じように適用される。具体的には、成熟鎖の21位がGまたはT(U)である場合、ゆらぎ塩基対が形成されるように、スター鎖の相対する位置は、それぞれT(U)またはGに変換される。成熟鎖が21位にGまたはT(U)以外の基をもつ場合、スター鎖は、標準的ワトソン−クリック塩基対が形成されるように設計される。
参照する熟成鎖の位置に相対するスター鎖の位置は、上記表1および表2に示される。例えば、miRNA−196a−2などのスキャホールドに挿入される標的配列の機能を高めるために、上記した追加条件の1つ以上の条件を式1または式2と組み合わせることができる。
ここで、多くの場合において、上記した工程が行われる順番は決定的なものではない。従って、例えば配列類をアルゴリズムによってスコア化し、その後、所望しない性質をもつシード類を除外するために高スコアの配列類をスクリーンすることができる。または、可能性のある配列類のリストを作成し、所望しない性質をもつシード類を除外するためにスクリーンし、続いて機能性標的配列を決めるために、残った配列類を前記アルゴリズムで評価することができる。
各々の式によって、様々な範囲にある可能性のある生のスコアが算出される。また、異なる式から算出されるスコアを、さらに比較可能で容易に評価できようにするために、数学的方法を用いて各々の式から求めた生スコアを標準化することが可能である。それぞれの式には、異なる標準化方程式が存在できる。標準化方程式は、全てのまたはほとんど全ての設計配列類について0−100の範囲でスコアを出すように選ばれることが好ましい。遺伝子サイレンシングを行うことを計画する場合、式によって算出された生スコアを比較することで、または、全ての式の間で、標準化したスコアを比較することで配列類を選択するべきである。
<アルゴリズムを使用しないで標的RNAの標的配列を選択する実施形態>
すぐ上で述べた実施形態では、例えば、特定のmiRNAスキャホールドに特有の様々な条件に合う配列について標的RNAをスキャンするためのアルゴリズムを用いている。このアルゴリズムによって決定した配列に完全に逆相補的な成熟鎖は、続いて、スキャホールドに導入される。従って、このアルゴリズムは、特定のスキャホールド内にある最も機能的と思われる配列類を選択する。一方、別の実施形態では、このようなアルゴリズムを使用することなしに標的RNA配列が選択される。このような実施形態では、選択された標的RNA配列に完全逆相補的となる成熟鎖が設計される。続いて、この成熟鎖は非天然存在型miRNAを形成するようにmiRNAスキャホールドに挿入される。標的RNA配列の完全逆相補配列となる成熟鎖の発現によって、標的RNAがRISCで切断されると、理論または作用機構に限定されることなく思われる。
すぐ上で述べた実施形態では、例えば、特定のmiRNAスキャホールドに特有の様々な条件に合う配列について標的RNAをスキャンするためのアルゴリズムを用いている。このアルゴリズムによって決定した配列に完全に逆相補的な成熟鎖は、続いて、スキャホールドに導入される。従って、このアルゴリズムは、特定のスキャホールド内にある最も機能的と思われる配列類を選択する。一方、別の実施形態では、このようなアルゴリズムを使用することなしに標的RNA配列が選択される。このような実施形態では、選択された標的RNA配列に完全逆相補的となる成熟鎖が設計される。続いて、この成熟鎖は非天然存在型miRNAを形成するようにmiRNAスキャホールドに挿入される。標的RNA配列の完全逆相補配列となる成熟鎖の発現によって、標的RNAがRISCで切断されると、理論または作用機構に限定されることなく思われる。
また、別の実施形態では、選択された標的RNA配列に一部だけが逆相補的となる成熟鎖が設計される。続いて、この成熟鎖は非天然存在型miRNAを形成するようにmiRNAスキャホールドに挿入される。このような成熟鎖のシード領域(2位−7位)は、標的RNA配列(類)の1つ以上の領域に完全に相補的であることが好ましいが、しかし、成熟鎖の残りの部分には、標的RNA配列に相補的ではない1つ以上の塩基類が含まれることが好ましい。このような成熟鎖が標的RNAに発現された場合、切断よりもむしろ翻訳減衰が起きると、理論または作用機構に限定されることなく思われる。
以前の研究から、翻訳減衰の経路によって遺伝子発現を効果的に調整するために、成熟鎖のシード領域と標的RNA(類)の領域(好ましくは、3’UTR)とが相補的なことが望ましいことが示された。さらに考慮してもよい1つ以上の追加パラメータには、1)特定の短配列(6ヌクレオチドなど)が、好ましくは、約10−50ヌクレオチド離れて標的RNAの3’UTR内で2回以上繰り返される標的RNA配列類を選択することが含まれる。このことにより、標的RNAに2つ以上の相補性をもつシード領域(2位−7位)を有する成熟鎖配列を設計できる。例えば、1つの成熟鎖が1つの3‘’UTRの2つ以上の領域を標的にできる。さらに、2)RNAi媒介翻訳減衰(例えば、AUに富む配列類)により遺伝子調節を促進するさらなるサイトと任意に結合する標的遺伝子内にある標的配列類を選択することを可能とし、3)成熟鎖の1位でAU塩基対を形成し、成熟鎖の位ではワトソン−クリック塩基対を形成することができる標的遺伝子配列を選択することを可能とする。このような考慮または他の設計を考慮することで、翻訳減衰メカニズムにより遺伝子調節を大きく促進することができる。
<非天然存在型miRNA類の発現および利用>
本発明の非天然存在型miRNA類は、プラスミド、および外在的配列あるいはホストゲノムに挿入する配列を保持するウイルスベクターを含む様々なベクター構築系において発現することが可能である。ここで、前記非天然存在型miRNA類には、式1または式2によって成熟鎖が合理的に設計されるmiRNA、式1または式2を用いて成熟鎖が選択されないmiRNA、およびshMIMICが含まれる。例えば、(A)塩基2−塩基19が式1により決められる、またはmiRNA−196a−2以外のmiR成熟鎖に由来する、および、(B)塩基20−塩基21が各々、miRNA−196a−2の21ヌクレオチド成熟鎖の内在性配列であるGである、21ヌクレオチド成熟鎖があるとする。この21ヌクレオチド成熟鎖を、次の配列をもつベクターインサートを生成するように、21ヌクレオチド スター鎖(TC−S1−S19)と並べて、miRNA−196a−2スキャホールドに導入してもよい。
5' TGATCTGTGGCT +[ M 1 -M 19 -GG] + GATTGAGTTTTGAAC+ [TC-S 1 -S 19 ] +AGTTACATCAGTCGGTTTTCG 3 ' 。 SEQ ID NO:24
この配列の逆相補配列は、適当なベクターにアニールおよびクローニング可能で、所望の遺伝子を長期にサイレンシングさせるなど標的RNAの機能性を低下させるために発現させることができる。ここで、21ヌクレオチドおよび22ヌクレオチド内在性miRNA−196a−2熟成鎖の両方が存在することを支持する証拠がある。従って、上記配列は、細胞内で発現する場合、21ヌクレオチド成熟鎖(M1−M19−GG)および/または21ヌクレオチド成熟鎖(M1−M19−GGG)を生成するように処理される。よって、上記配列において下線で示したGは、miRNA−196a−2スキャホールドの一部であるか、または、成熟鎖の一部であってよい。
本発明の非天然存在型miRNA類は、プラスミド、および外在的配列あるいはホストゲノムに挿入する配列を保持するウイルスベクターを含む様々なベクター構築系において発現することが可能である。ここで、前記非天然存在型miRNA類には、式1または式2によって成熟鎖が合理的に設計されるmiRNA、式1または式2を用いて成熟鎖が選択されないmiRNA、およびshMIMICが含まれる。例えば、(A)塩基2−塩基19が式1により決められる、またはmiRNA−196a−2以外のmiR成熟鎖に由来する、および、(B)塩基20−塩基21が各々、miRNA−196a−2の21ヌクレオチド成熟鎖の内在性配列であるGである、21ヌクレオチド成熟鎖があるとする。この21ヌクレオチド成熟鎖を、次の配列をもつベクターインサートを生成するように、21ヌクレオチド スター鎖(TC−S1−S19)と並べて、miRNA−196a−2スキャホールドに導入してもよい。
5' TGATCTGTGGCT +[ M 1 -M 19 -GG] + GATTGAGTTTTGAAC+ [TC-S 1 -S 19 ] +AGTTACATCAGTCGGTTTTCG 3 ' 。 SEQ ID NO:24
この配列の逆相補配列は、適当なベクターにアニールおよびクローニング可能で、所望の遺伝子を長期にサイレンシングさせるなど標的RNAの機能性を低下させるために発現させることができる。ここで、21ヌクレオチドおよび22ヌクレオチド内在性miRNA−196a−2熟成鎖の両方が存在することを支持する証拠がある。従って、上記配列は、細胞内で発現する場合、21ヌクレオチド成熟鎖(M1−M19−GG)および/または21ヌクレオチド成熟鎖(M1−M19−GGG)を生成するように処理される。よって、上記配列において下線で示したGは、miRNA−196a−2スキャホールドの一部であるか、または、成熟鎖の一部であってよい。
好適なウイルスベクターには、レンチウイルス(HIV、FIVなど) ベクター、レトロウイルス ベクター、アデノウイルス ベクター、アデノ関連 ベクター、およびラビエス ベクターなどがあるがこれに限定されるものではない。これらのベクター全てにおいて、非天然存在型miRNAは非コードRNA類(ポリメラーゼIIIプロモーターなど)として転写されるか、または、ポリメラーゼIIプロモーターにより転写されるメッセンジャーRNAと関連付けることができる。
ある実施形態では、プロモーターは組織特異的なプロモーターである。また、別の実施形態では、プロモーターはtetプロモーターまたがReoswitchTMなどの調節可能なプロモーターである。プロモーター配列は、標的にするホスト由来であるか、または、別の生物のゲノムから採取できる。従って、例えば、プロモーターはCMV、HIV、FIV、またはRSVプロモーター配列(LTR(Long Terminal Repeat)プロモーターなど)などのウイルスプロモーターが可能である。非天然存在型miRNAをコードする配列類を、ベクター系と関連する他の要素を考慮して様々な位置に置くことができる。例えば、非天然存在型miRNAをコードする配列類を、ポリメラーゼIIプロモーターから発現され遺伝子の5’および/または3’UTR、または、遺伝子の1つ以上のイントロンに挿入される遺伝子に関連させることができる。好適な実施形態では、非天然存在型miRNAをコードする配列類は、蛍光レポーター(GFP、YFP、RFP、およびBFPなど)、酵素的レポ−ター(ルシフェラーゼなど)、または、薬物耐性マーカー(プロマイシンなど)、または、その発現が細胞の生理学的性質を著しくは変化させない他の遺伝子類を含む、マーカーおよび/または遺伝子と関連する。また、別の例では、非天然存在型miRNAの発現を、ポリメラーゼIIプロモーターから非コード配列として転写された遺伝子の発現に関連させないようにすることが可能である。また、ある例では、前記調節により、組織特異的調節可能な発現系を生成するために、調節可能なプロモーター(例えば、PTET)を組織特異的プロモーターと組み合わせるなど、上記複数の要素を組み入れることができる。
ある実施形態では、プロモーターは組織特異的なプロモーターである。また、別の実施形態では、プロモーターはtetプロモーターまたがReoswitchTMなどの調節可能なプロモーターである。プロモーター配列は、標的にするホスト由来であるか、または、別の生物のゲノムから採取できる。従って、例えば、プロモーターはCMV、HIV、FIV、またはRSVプロモーター配列(LTR(Long Terminal Repeat)プロモーターなど)などのウイルスプロモーターが可能である。非天然存在型miRNAをコードする配列類を、ベクター系と関連する他の要素を考慮して様々な位置に置くことができる。例えば、非天然存在型miRNAをコードする配列類を、ポリメラーゼIIプロモーターから発現され遺伝子の5’および/または3’UTR、または、遺伝子の1つ以上のイントロンに挿入される遺伝子に関連させることができる。好適な実施形態では、非天然存在型miRNAをコードする配列類は、蛍光レポーター(GFP、YFP、RFP、およびBFPなど)、酵素的レポ−ター(ルシフェラーゼなど)、または、薬物耐性マーカー(プロマイシンなど)、または、その発現が細胞の生理学的性質を著しくは変化させない他の遺伝子類を含む、マーカーおよび/または遺伝子と関連する。また、別の例では、非天然存在型miRNAの発現を、ポリメラーゼIIプロモーターから非コード配列として転写された遺伝子の発現に関連させないようにすることが可能である。また、ある例では、前記調節により、組織特異的調節可能な発現系を生成するために、調節可能なプロモーター(例えば、PTET)を組織特異的プロモーターと組み合わせるなど、上記複数の要素を組み入れることができる。
また、特定のベクター構築に関連した非天然存在型miRNA類の数も変えることができる。ある実施形態では、1つの非天然存在型miRNAは1つのベクターから発現する。また、別の実施形態では、2つ以上の非天然存在型miRNA類(プールなど)が1つの1つのベクターから発現する。2つ以上の非天然存在型miRNA類が発現する場合、これら非天然存在型miRNA類は互いに関連する必要はなく、1つの転写(例えば、同じ3’UTRにある2つの非天然存在型miRNA類)に関連させることができる。または、2つの別々の転写に関連させることができる(例えば、2つの非天然存在型miRNA類が、2つの関連しない転写に関連し発現される)。1つのベクターから複数の非天然存在型miRNA類が発現する場合、非天然存在型miRNA類は同じもの(例えば、非天然存在型miR−196a−2 miRNA類の2コピー)であるか、または、異なるものであることが可能である。異なるものである場合の例としては、非天然存在型miR−196a−2 miRNAの1コピーと非天然存在型miR−204 miRNAの1コピー、または、同じ成熟鎖だが異なるスキャホールドをもつ2つのshMIMICS、または、shMIMICとランダムに選ばれた成熟鎖か合理的に設計された成熟鎖のどちらか1つをもつ非天然存在型miRNA、などが含まれる。さらに、非天然存在型 miRNA類は、1つの遺伝子産物を標的にする配列類のプールを効果的にもつ、単一の標的RNAを標的にできる。または、非天然存在型 miRNA類は複数の遺伝子を標的にすることが可能である(複数遺伝子標的)。プーリングおよび複数遺伝子標的の両者ともに、本発明の非天然存在型 miRNA類を用いて別の手段により達成することができる。具体的には、1つ以上の標的遺伝子を標的にする複数の非天然存在型 miRNA類を、複数のベクター類に挿入し、その後、組み合わせ(混合して)、所望の細胞内に、1)トランスフェクション、または、2)トランスデュースすることができる。
非天然存在型miRNA類をコードするベクター構築体類は、公知のまたは本発明の記載から当業者が本発明との関連で有用とするどの方法を用いて細胞に導入してもよい。これらの方法には、任意の方法によるトランスフェクション、例えば、DEAE−Dextran、リン酸カルシウム、カチオン性脂質/リポソーム、ミセル、圧力法、マイクロインジェクション、電気泳動、イムノポレーション、ウイルスベクターの使用、コスミド、バクレリオファージ、細胞融合、および特定のコンジュゲードまたはリガンドとの結合などを用いる方法があるが、これらに限定されるものではない。
非天然存在型miRNA類がウイルスを用いて細胞に輸送される場合、ベクター構築体はチトプラズムで保存できる。または、レンチウイルスなどのホストゲノムに統合されて発現できる。こうしたベクターは、先のウイルスをパッキングするのに必要な配列類を頻繁に含むが、しかし、伝染性粒子の生成を防ぐために「ヘルパー」プラスミドによってもたらされる機能を欠く。また、ウイルス系が用いられる場合、構築体を発現させるプロモーターを変えることによって、つまり、構築体の発現レベルを変えることによって、構築体の発現レベルを操作することができる。または、伝染の多様性(MOI)を調節することで、効果的には、各々の細胞に置かれた発現カセットのコピーの数を変えることによって、発現レベルを変えることができる。
別の実施形態では、本発明は、少なくとも1つの非天然存在型miRNA類からなるキットを提供する。
また、別の実施形態では、本発明は、非天然存在型miRNA類をコードする少なくとも1つのベクター構築体からなるキットを提供する。
また、別の実施形態では、本発明は、少なくとも1つのmiRNAスキャホールドからなるキットを提供する。前記miRNAスキャホールドは、miRNAスキャホールドに成熟鎖およびスター鎖配列をクローニングし、続いて得られた非天然存在型miRNA類を細胞内で発現させることで、shMIMICSを含む複数の異なる非天然存在型miRNA類を生成させるために用いることができる。
本発明のmiRNAスキャホールド類、非天然存在型miRNA類、および方法は、基礎研究に限定されない、医薬品の発見と開発、診断、および治療を含む様々な用途に用いてよい。それぞれの場合において、miRNAスキャホールドに成熟鎖配列を導入することにより生成される非天然存在型miRNAは、所望の遺伝子により生成したmRNAなどの標的RNAの機能性を低下させるために用いられる。また、研究を準備するにあたり、遺伝子産物が医薬品の発見または開発の標的であるかどうかを確認するために、本発明の構成物および方法を用いてもよい。
RNAi経路で機能するように、本発明の非天然存在型miRNA内に配置された成熟鎖配列類の機能は、特定の遺伝子によって生成したmRNAなどの標的RNAの配列に依存し、標的RNAが導入される種には依存しないので、本発明の構成物および方法は、広範囲の種にわたる標的遺伝子に用いてよい。このような種としては、ヒト、イヌ、ウマ、ネコ、ウシ、マウス、ハムスター、チンパンジー、およびゴリラなどの全ての哺乳類の種、および、他の種やバクテリア、ウイルス、昆虫、植物、虫類などの生物が含まれるが、これらに限定されるものではない。
また、本発明の構成物および方法は、広範囲の遺伝子類をサイレンシングするために用いることができる。このような遺伝子類には、ヒトゲノムの約45,000の遺伝子が含まれるが、これらに限定されるものではない。先に述べた生物のゲノム中にある全ての遺伝子類とともに、ヒトゲノム遺伝子類が、糖尿病、アルツハイマー、癌などの疾患に関わるケースに特に係る。
また、別の適用としては、特定のファミリーの遺伝子類(キナーゼなど)、特定の経路(細胞サイクルの調節など)に関わる遺伝子類、または完全なゲノム類(例えば、ヒト、ラット、マウス、C.elegans,Drosophiaゲノムなど)に向けられた、非天然存在型miRNA類を提供する。遺伝子類のRNA産物に少なくとも一部相補的な成熟鎖配列類を有する非天然存在型miRNA類を用いて、集めた遺伝子の各々をノックダウンすることで、遺伝子ファミリーの各メンバー、経路の各メンバー、または、ゲノムの各遺伝子が特定の生物学的機能に寄与する程度を、研究者は直ちに評価することが可能となる。
また、本発明の構成物および方法を、所望の病気または疾患の原因または要因と思われる所望の標的RNAの活性を弱めることにより、病気または疾患状態を一時的または長い期間、生物に誘発するのに必要であるRNA干渉法に適用してもよい。所望の標的RNAの活性を増強することで、病気または疾患を悪化させたり、またはケースにより、所望の病気または疾患を改善したり治癒させてもよい。同様に、所望の標的核酸の活性を弱めることで、病気または疾患を悪化させたり、またはケースにより、所望の病気または疾患を改善したり治癒させてもよい。所望の標的RNAは、ゲノムまたはクロモソ−ムの核酸類、または、ウイルスの核酸類などのクロモソーム外の核酸類を有することができる。
また、本発明の構成物および方法を、予防薬および治療薬など、RNA干渉法の応用に用いてもよいこのような応用としては、所望の特定の標的RNAを操作することで、調節可能な病気または疾患をもつと疑われる生物を、好適なスキャホールドを発現させる系に配置された標的配列類を服用することによって治療さする。この治療結果は、特定の病気または疾患を、改善、緩和、予防、および/または、診断するものであってよい。標的配列類は、薬学的に許容されるキャリア、希釈剤、または輸送システム(例えば、ウイルス)を用いて薬学的に許容される方法で服用されることが好ましい。
また、本発明の成熟非天然存在型miRNA類は、静脈、筋肉、皮膚、皮下、鼻、経口、直腸などを経由する輸送経路により、または点眼により、または所望の標的核酸がある臓器、組織または細胞などの有効な部位に薬剤を放出する装置を組織移植することによって、服用することが可能である。
また、本発明は、非天然存在型miRNAによって標的にされる遺伝子が不適当に発現されることを特徴とする病気を治療する医薬品を製造することに、非天然存在型miRNAを利用することを開示する。
本発明の好適な実施形態を、実施形態を変えるまたは別の実施形態を示しながら、図で説明し、詳細に述べる。本発明が示し、記載し、図示する内容により、形態や詳細における同じような変換を、本発明の精神および範囲から離れることなしに行われてもよく、本発明の範囲が、先行技術によって除かれる内容を別にすれば、請求項にのみ限定されるものであることが、当業者によって理解されるべきである。さらに、ここに記載されるような本発明が、ここに開示される特定の要素がなくとも、好適に実施されるものである。
本出願に引用される全ての引用文献は、ここに記載される内容に合致して本明細書中にその全体を引用するものである。
次に記載する実施例は、本発明を例示する目的にのみ用いられるものであり、本発明の範囲を限定する目的に用いるものではない。
次に記載する専門用語は、siRNAサイレンシング機能を比較および報告するために用いた。例えば、「F」に続く数字は、最小ノックダウンの程度を示した。例えば、F50は、少なくとも50%ノックダウンであることを意味し、F80は、少なくとも80%ノックダウンであることを示す。本研究では、F50 RNA以下の全ての値は、非機能性であると見なした。
<一般的技術>
全体のゲノムDNA抽出:全HeLaゲノムDNAはDNeasy Genomic DNA単離キットを用いて抽出した。DNAの全体の完全性は、エチジウムブロミドを用いて着色した0.8%アガロースゲルで確認した。
<ゲノムDNAに由来するmiRNA類のPCR増幅>
PCRは、2重ルシフェラーゼ系での試験用に様々なmiRNAを増幅するために使用した。Quiagen Tag PCR Master Mix(カタログ番号201443)を用いた10−100ng HeLaゲノムDNAおよび各プライマー10μMから、天然miRNA類を増幅した。PCRパラメータ:最初の変性を94℃で4分間、94℃で15秒間、50−60℃で30秒間、30サイクルを72℃で45秒間、最終伸長を72℃で2分間。以下の表3に増幅に用いた配列類を示した。
PCRは、2重ルシフェラーゼ系での試験用に様々なmiRNAを増幅するために使用した。Quiagen Tag PCR Master Mix(カタログ番号201443)を用いた10−100ng HeLaゲノムDNAおよび各プライマー10μMから、天然miRNA類を増幅した。PCRパラメータ:最初の変性を94℃で4分間、94℃で15秒間、50−60℃で30秒間、30サイクルを72℃で45秒間、最終伸長を72℃で2分間。以下の表3に増幅に用いた配列類を示した。
プラーマセットのうち2つのプライマー(miR338とmiR135a−2)がそれぞれのサイトの増殖ができなかった。残りのスキャホールド類については、PCR産物は、ゲル精製、SpeI/BgIII(NEB)で処理、人工イントロンを含むGFPで高修飾したpCMV−Tag4のMCSにクロ−ニングした。クローニングの成功をシークエンシングで確認した。このような方法を用いた結果、GFPのATG開始サイトの人工イントロン下流内に、miRNA類が局所に限定して配置された。図4参照。
<psi Check 2重ルシフェラーゼ レポーター 構築体>
自身のプロモーターおよびポリ(A)追加サイトをもつ、ヒト化ホタルルシフェラーゼ遺伝子(hluc)およびヒト化ウミシイタケルシフェラーゼ遺伝子(hRluc)を有する、2重ルシフェラーゼプラスミド(psiCHECKTM−2ベクター)はPromega(カタログ番号C8021)から得た。逆相補標的配列類は、hRluc遺伝子3’UTRのクローニングサイトにあるXhol−NotI制限領域の間に挿入した。挿入した配列類は、制限領域に即して挿入されるようにOperonから並べられた。Dual−GloTMルシフェラーゼアッセイシステム(Progma、カタログ番号E2980)を用い、手引書の手順を少し変えて、ホタルおよびウミシイタケルシフェラーゼ活性を測定した。細胞を分解するとき、50μLのホタルルシフェラーゼおよび50μLのウミシタケルシフェラーゼを加える前に培地を細胞からアスピレーションした。
自身のプロモーターおよびポリ(A)追加サイトをもつ、ヒト化ホタルルシフェラーゼ遺伝子(hluc)およびヒト化ウミシイタケルシフェラーゼ遺伝子(hRluc)を有する、2重ルシフェラーゼプラスミド(psiCHECKTM−2ベクター)はPromega(カタログ番号C8021)から得た。逆相補標的配列類は、hRluc遺伝子3’UTRのクローニングサイトにあるXhol−NotI制限領域の間に挿入した。挿入した配列類は、制限領域に即して挿入されるようにOperonから並べられた。Dual−GloTMルシフェラーゼアッセイシステム(Progma、カタログ番号E2980)を用い、手引書の手順を少し変えて、ホタルおよびウミシイタケルシフェラーゼ活性を測定した。細胞を分解するとき、50μLのホタルルシフェラーゼおよび50μLのウミシタケルシフェラーゼを加える前に培地を細胞からアスピレーションした。
細胞生育力は、alamarBlueRアッセイ(BioSource Intl,Inc)を用いて2重プレート上で測定した。コントロールおよび実験で処理した細胞の細胞生育力は、15%以内であった。
mRNA定量測定が必要な実験については、1X分解混合物中細胞を分解し、分岐DNA(bDNA)アッセイ(QuantiGeneRスクリーニングキット、カタログ番号QG−000−050、Promega)によってmRNA定量を行った。標的遺伝子類の分岐DNAプローブはPanomicsおよび社内で設計した。
ルシフェラーゼ、alamarBlueおよびbDNAアッセイは、業者推薦プログラムを用い、Wallac Victor 1420多重カウンター(Perkin Elmer)により測定した。
<細胞培養およびトランスフェクション>
トランスフェクションを行う1日前、HeLa細胞を、無抗体の10%ウシ胎仔血清(FBS)を加えたDulbecco修飾Eagle培地(DMEM)中で、1ウエルあたり約10,000細胞の細胞密度で96穴プレートにプレーティングした。トランスフェクション当日、適当な標的配列類を含むpsiCheck2重ルシフェラーゼプラスミド、スキャホールド構築体を発現するコントロールおよび実験用プラスミド、標的配列を標的するsiRNA類(100nM)、Lipofectamine2000などの脂質輸送試薬類の混合物を調製した。この混合物を、当業者によく知られたトランスフェクション条件を用いて、細胞内に導入した。
トランスフェクションを行う1日前、HeLa細胞を、無抗体の10%ウシ胎仔血清(FBS)を加えたDulbecco修飾Eagle培地(DMEM)中で、1ウエルあたり約10,000細胞の細胞密度で96穴プレートにプレーティングした。トランスフェクション当日、適当な標的配列類を含むpsiCheck2重ルシフェラーゼプラスミド、スキャホールド構築体を発現するコントロールおよび実験用プラスミド、標的配列を標的するsiRNA類(100nM)、Lipofectamine2000などの脂質輸送試薬類の混合物を調製した。この混合物を、当業者によく知られたトランスフェクション条件を用いて、細胞内に導入した。
<実験設計およびデータ分析>
実験は全てトリプリケートで行った。レセプタープラスミドに対する非特異的影響を評価するために、実験結果は全て標準化比(Rluc/Fluc)標準化として表わした。この比は、miRNAリポータープラスミド(Rluc/Fluc)miRNAを、リポータープラスミドとコトランスフェクションさせた非標的配列で割って算出した、ホタツルシフェラーゼ発現に対するウミシタケルシフェラーゼ発現の比である。このレポータープラスミドから得られた最大値は配列によって変化する。1周辺の値はmiRNA機能が低いことを示すが、一方、0に近い値は低miRNA機能が高いことを示す。データは3つのウエルの平均値として報告し、誤差バーは、標準化ファクターでスケール化された、実験から得た3つの比(Rluc/Fluc)コントロールの標準偏差を示す。これらの比は標準的分布に従わないが、標準偏差値はデータの良い変化値を示すものと考える。
実験は全てトリプリケートで行った。レセプタープラスミドに対する非特異的影響を評価するために、実験結果は全て標準化比(Rluc/Fluc)標準化として表わした。この比は、miRNAリポータープラスミド(Rluc/Fluc)miRNAを、リポータープラスミドとコトランスフェクションさせた非標的配列で割って算出した、ホタツルシフェラーゼ発現に対するウミシタケルシフェラーゼ発現の比である。このレポータープラスミドから得られた最大値は配列によって変化する。1周辺の値はmiRNA機能が低いことを示すが、一方、0に近い値は低miRNA機能が高いことを示す。データは3つのウエルの平均値として報告し、誤差バーは、標準化ファクターでスケール化された、実験から得た3つの比(Rluc/Fluc)コントロールの標準偏差を示す。これらの比は標準的分布に従わないが、標準偏差値はデータの良い変化値を示すものと考える。
<高性能miRNAスキャホールド類の同定>
高機能性miRNAスキャホールド類を同定するために、10個の異なるmiRNAをゲノムDNA(miR−126、204、196a−2、−30c−1、−26b、−30a、−374、−196a−1、−526、および−486を含む)からPCR増幅し、GFPの人工イントロンのSpeI/BgIIIサイトにクロ−ニングした(図4A−図E参照)。並行して、hRlucの3’UTRにある標的サイト(逆相補的)を含む2重ルシフェラーゼリポーターを構築した(図4Fおよび表4参照)。人口miRNA発現ベクトルおよび2重ルシフェラーゼレポーターベクターをコードするプラスミドは、標準的な鎖方向トランスフェクション技術によるLipofectamine 2000(Invitrogen, 0.2μl/ウエル)を用いて、HeLa細胞(96穴プレートの1ウエル中10K細胞)中にコトランスフェクションした。さらに48時間後、ルシフェラーゼレポーターのノックダウンレベルを測定するためにアッセイした。
高機能性miRNAスキャホールド類を同定するために、10個の異なるmiRNAをゲノムDNA(miR−126、204、196a−2、−30c−1、−26b、−30a、−374、−196a−1、−526、および−486を含む)からPCR増幅し、GFPの人工イントロンのSpeI/BgIIIサイトにクロ−ニングした(図4A−図E参照)。並行して、hRlucの3’UTRにある標的サイト(逆相補的)を含む2重ルシフェラーゼリポーターを構築した(図4Fおよび表4参照)。人口miRNA発現ベクトルおよび2重ルシフェラーゼレポーターベクターをコードするプラスミドは、標準的な鎖方向トランスフェクション技術によるLipofectamine 2000(Invitrogen, 0.2μl/ウエル)を用いて、HeLa細胞(96穴プレートの1ウエル中10K細胞)中にコトランスフェクションした。さらに48時間後、ルシフェラーゼレポーターのノックダウンレベルを測定するためにアッセイした。
図5に本研究結果を示すが、いくつかのmiRNAスキャホールドは他のスキャホールドよりも機能性か高いことを示す。構築体の半数は、レポーター構築体を有意にサイレンスすることができないため、その後の研究から除外した。miR−30a、−374、−196a1、−526、および−486は、全て80%以下のレポーター構築体サイレンシングであった。また、miR−126の研究から、5’および3’鎖としてそれぞれ示される成熟鎖およびスター鎖の両者、およびヘパリンが機能性であることを見出した。成熟鎖およびスター鎖の両者が活性をもつことは、ある応用には好適かもしれないが、しかし、この構築体の実験はその後行わなかった。残りの3つのmiRスキャホールド(−204、−26b、および−196a)は、2重ルシフェラーゼ構築体を80%以上サイレンシングし、高機能性であると同定された。興味深いことに、miR−196a−2と同じ成熟鎖をもつmiR−196a−1が、最も最適化されていないスキャホールドでることが同定された。このことは、成熟miR配列を囲む配列がDrosha/Dicerプロセスで重要な役割を果たし、こうした効果がmiRNAに大きな影響を与えているかもしれないことを示唆している。
<外部配列クロ−ニングを可能にするmiRNAスキャホールド配列類の修飾>
配列類を輸送および標的化するmiRNAスキャホールドの重要な特性は、スキャホールド内にクロ−ン配列を導入して機能性を保持する能力である。このことを実現するために、標準的な分子生物学的技術を用い、構築体の中に制限領域を組み込むために、実施例1で同定した3つの高機能性スキャホールド(miR−26b、196a2、および−204)を修飾した。その後、この修飾が成熟鎖の活性またはスター鎖活性を変化させたかどうかを測定するために、成熟標的鎖に逆相補的な配列を含む2重ルシフェラーゼレポーターを用いて、各構築体を試験した。また、miR−26bおよびmiR−204について、BlpIおよびSacI制限領域を構築体に導入するために、ヌクレオチド修飾を行った(図6(a)、(b)上部参照)。miR−196a−2については、天然BlpI領域が既に構築体内にあるので、第2制限領域(SacI、ScaL、およびXbaI)を合わせて試験した(図6(c)上部および下部参照)。
配列類を輸送および標的化するmiRNAスキャホールドの重要な特性は、スキャホールド内にクロ−ン配列を導入して機能性を保持する能力である。このことを実現するために、標準的な分子生物学的技術を用い、構築体の中に制限領域を組み込むために、実施例1で同定した3つの高機能性スキャホールド(miR−26b、196a2、および−204)を修飾した。その後、この修飾が成熟鎖の活性またはスター鎖活性を変化させたかどうかを測定するために、成熟標的鎖に逆相補的な配列を含む2重ルシフェラーゼレポーターを用いて、各構築体を試験した。また、miR−26bおよびmiR−204について、BlpIおよびSacI制限領域を構築体に導入するために、ヌクレオチド修飾を行った(図6(a)、(b)上部参照)。miR−196a−2については、天然BlpI領域が既に構築体内にあるので、第2制限領域(SacI、ScaL、およびXbaI)を合わせて試験した(図6(c)上部および下部参照)。
miR−26bについては、SacI領域の導入は、成熟鎖の機能性全体にほとんどまたは全く影響を与えなかった(図6(a)、下部参照、約85−90%機能性を示す)。また、追加したBlpI領域の修飾(BlpI/SacI)は、機能性全体に少し影響を与え、成熟鎖によるサイレンシングを約80%に減らした。また、BlpI/SacIを組み合わせた修飾は、スター鎖活性をさらに制限した。以上の研究結果から、miR−26bスキャホールドに外部配列類をクローニングするのに使用可能な、制限領域の相補的な1組(BlpI/SacI)を同定した。
miR−204については、SacIまたはSacI/BlpIどちらの領域の導入も、成熟鎖活性に影響を与えなかった(図6b、下部参照)。miR−26b構築体で見られたように、2つの制限領域に導入するスキャホールドの修飾は、スター鎖の機能性を抑制した(約60%サイレンシング→約40%サイレンシング)。従って、以上の研究結果から、2つの目的が達成された。第1に、miR−204 スキャホールドに外部配列類をクローニングするのに使用可能な、制限領域の相補的1組を同定した。第2に、miR−204スター鎖の機能性をさらに制限する修飾を見出した。
miR−196a−2スキャホールドに合う制限領域の組み合わせは、問題があることを見出した(図6(c)参照)。図6(d)に示すように、ScaI領域(または、SacIとScaI領域との組み合わせ)を加えた場合、成熟鎖活性を著しく低下させた。ScaI+およびScaI+/SacI+の両構築体は、スター鎖活性を高めることを示した。スター鎖活性の促進は好ましくないので、この制限領域の組み合わせは行わないことにした。
幸い、SacI領域の導入だけが成熟鎖活性に影響をほとんど与えずに、さらにスター鎖の機能性を抑制した(図6(d)、40%サイレンシング→20%サイレンシング)。そこで、miR−204の場合と同様に、2つの別々の目標が達成された。第1に、miR−196a−2スキャホールドに外部配列類をクローニングするのに使用可能な、制限領域の相補的1組を同定した。第2に、miR−196a−2スター鎖の機能性をさらに制限する修飾を見出した。
<外部配列類を許容するmiRNAスキャホールドの同定>
3つの好適なmiRNAスキャホールドの中で、どのスキャホールドが最も外部配列類を許容するのかを測定するために、本研究で「ウオーク」GADPH標的配列類を各スキャホールド内に埋め込み、GFPの人工イントロン内にクローニングした。ここで、ウオークは、2bpだけシフトした各配列に5’末端をもち、長さが21bpである配列類より構成される(図7(a)参照)。3つのベクターすべての場合において、各内在性スキャホールド類に存在する天然の2位構造(例えば、ブルジやミスマッチ構造)を保持するように、挿入を設計した。また、単純なヘパリン構造などの2次構造をもたないmiR−196a−2スキャホールドに埋め込んだ各配列によって構成される第4のウオークを、機能性における2次構造の重要性を理解するために試験した。3つのスキャホールドから得られた結果を、細胞内に等価な合成siRNAをトランスフェクションしたときに得られた結果と比較した。また、psiCheck(2重ルシフェラーゼ)レポーターに埋め込んだGAPDH標的配列を、図7(b)に示す。
3つの好適なmiRNAスキャホールドの中で、どのスキャホールドが最も外部配列類を許容するのかを測定するために、本研究で「ウオーク」GADPH標的配列類を各スキャホールド内に埋め込み、GFPの人工イントロン内にクローニングした。ここで、ウオークは、2bpだけシフトした各配列に5’末端をもち、長さが21bpである配列類より構成される(図7(a)参照)。3つのベクターすべての場合において、各内在性スキャホールド類に存在する天然の2位構造(例えば、ブルジやミスマッチ構造)を保持するように、挿入を設計した。また、単純なヘパリン構造などの2次構造をもたないmiR−196a−2スキャホールドに埋め込んだ各配列によって構成される第4のウオークを、機能性における2次構造の重要性を理解するために試験した。3つのスキャホールドから得られた結果を、細胞内に等価な合成siRNAをトランスフェクションしたときに得られた結果と比較した。また、psiCheck(2重ルシフェラーゼ)レポーターに埋め込んだGAPDH標的配列を、図7(b)に示す。
図7(c)は合成19bp siRNAとして細胞内に導入されたときのウオーク中の各配列の機能性を示す。先に見られたように、標的siRNAの位置のわずかな変化が、機能性に非常に大きな影響を与えることができるこれと同じ配列類が、miR−26b、miR−204、およびmiR−196a−2に導入されて発現構築体として輸送されたとき、miR−204およびmiR−196a−2の2つのスキャホールドは、miR−26bスキャホールドよりも高い機能性レベルを示す(図7(d),(e),(f)参照)。興味深いことに、miR−196a−2構造に導入した配列類から2次構造を全て削除した場合、機能性が大きく抑制されることを見出した(図7(g)参照)。並べて比較すると、miR−196a−2およびmiR−204スキャホールドはmiR−26bスキャホールドよりもより多くの配列で機能性をもつことが示された(図7(h)参照)。また、これらの発見から、外部配列を輸送するのに3つのスキャホールド全てが有用であることが示され(最も好適になものとしてはmiR−196a−2およびmiR−204スキャホールド)、2次構造を保持することは最適の機能性のために好ましいことが示された。
<好適な標的配列類の分析>
miR−196a−2GAPDHウオークからの高機能性(>70%)配列類を、位置特異的傾向を同定するために評価した。この評価を行ったとき、直ちに、成熟鎖1位の「U」(この位置をコードするDNAでは「T」)が、外部遺伝子類を標的にする高機能性配列類に特徴的であることが明らかになった。この理由から、この条件が最適な機能性をもつのに好ましいと、先ず同定された。5位および6位には、TおよびAがそれぞれ好適であった。7位には、この位置にGをもつ配列類はほとんどなかった(図8(a)参照)。内在性miR−196a−2内でミスマッチする位置である12位には、「A」が少々、「T」がかなり存在した。13位にも「T」が多くあることが機能性配列類で観察された。このように、特定のヌクレオトド類について位置特異的な傾向が同定された。
miR−196a−2GAPDHウオークからの高機能性(>70%)配列類を、位置特異的傾向を同定するために評価した。この評価を行ったとき、直ちに、成熟鎖1位の「U」(この位置をコードするDNAでは「T」)が、外部遺伝子類を標的にする高機能性配列類に特徴的であることが明らかになった。この理由から、この条件が最適な機能性をもつのに好ましいと、先ず同定された。5位および6位には、TおよびAがそれぞれ好適であった。7位には、この位置にGをもつ配列類はほとんどなかった(図8(a)参照)。内在性miR−196a−2内でミスマッチする位置である12位には、「A」が少々、「T」がかなり存在した。13位にも「T」が多くあることが機能性配列類で観察された。このように、特定のヌクレオトド類について位置特異的な傾向が同定された。
続いて、各2次構造の重要性を同定する研究をさらに行った。1位に見られたGUゆらぎ塩基対のミスマッチを置換すると、全体の機能性に有害であることが観察された。同様に、12位に見られたミスマッチのサイズを12位および13位に伸ばすと、やはり有害であることを見出した。
機能性および非機能性配列類の分析から、機能性とGC含有量との間に強い相関があることを見出した。miR−196a−2GAPDHウオークで試験した配列類から得られた、全体のGC含有量と機能性との比較から、一般的に、最も高機能的な配列類は、GC含有量が少ないことが示された。図8(b)に示すように、10Gまたは10Cヌクレオチド以下のGCをもつ25個の配列類のなかで、18個の配列類(77%)が50%以上のサイレンシングを示す。この結果は、miR−196a−2スキャホールド内に挿入する外部配列類を設計する場合、全体のGC含有量を考慮するべきであることを示唆している。
<siRNAアルゴリズムとshRNAアルゴリズムとの比較>
miR−196a−2スキャホールドに挿入する外部配列類を用いて効果的に標的化できる標的サイトを同定できるアルゴリズムを開発するために、先の実施例で得られた結果を使用した(式1、式2および関連する記載内容参照)。miR−196a−2アルゴリズムおよびsiRNAを設計するのに用いられたアルゴリズムを用いて(米項特許出願第2005/0255487号明細書参照(出願番号10/940892、2004年9月14日出願)、CDC2遺伝子内に同定された標的サイトを並べて比較した結果、ほとんど重なり合わない異なる配列類をこれら2つのアルゴリズムが同定することが分かった(図9(a)参照)。
miR−196a−2スキャホールドに挿入する外部配列類を用いて効果的に標的化できる標的サイトを同定できるアルゴリズムを開発するために、先の実施例で得られた結果を使用した(式1、式2および関連する記載内容参照)。miR−196a−2アルゴリズムおよびsiRNAを設計するのに用いられたアルゴリズムを用いて(米項特許出願第2005/0255487号明細書参照(出願番号10/940892、2004年9月14日出願)、CDC2遺伝子内に同定された標的サイトを並べて比較した結果、ほとんど重なり合わない異なる配列類をこれら2つのアルゴリズムが同定することが分かった(図9(a)参照)。
この検討後、miR−196a−2アルゴリズムおよびsiRNAアルゴリズムを、MAPK1およびEGFRの2つの遺伝子に適用した(図9(b)−(c)参照)。続いて、標的配列類を、先に記載した制限領域を用いてmiR−196a−2スキャホールドにクローニングし、好適な2重ルシフェラーゼレポーター構築体並べてHeLa細胞にコトランスフェクションした(標的配列類については図9(b)(c)参照)。図9(d9にその結果を示す。EGFRについては、選択した5つのクロ−ンの中で、2つだけが80%を超える遺伝子ノックダウンを示した。対照的に、新しいmiR−196a−2アルゴリズムにより選択した5つのクロ−ンの中で、4つのクロ−ンが>80%の遺伝子ノックダウンを示した。MAPK1については、siRNAアルゴリズムにより選択した4つの配列類の中で、3つの配列類が>80%の遺伝子ノックダウンを示した。対照的に、新しいmiR−196a−2アルゴリズムにより選択した5つのクロ−ン全てが、>80%の遺伝子ノックダウンを示した。
miR−196a−2設計アルゴリズムの有効性をさらに試験した結果、CDC2(NM_001786)、CD28(NM_06139)、CD69(NM_001781)、およびLAT(NM_014387)に対する標的配列類を設計し、miR−196a−2スキャホールドにクローニングして、その後、2重ルシフェラーゼアッセイを用いて標的遺伝子をノックダウンする能力を試験した。これらの研究結果を、図9(e)に示す。miR−196a−2アルゴリズムを用いて設計した25個の配列類の中で、22個の配列類(88%)が75%を超えるサイレンシングを示した。
標的を十分にノックダウンできなかった構築体(例えば、<50%、Zap70、図9(f)に標的配列を示す)を詳細に研究した結果、ここで開示したアルゴリズムを用いて選択した数多くの配列類は、特に成熟鎖のシード領域内に一連のGおよびCを含むことが明らかになった(図9(g)参照)。続いて行った機能性標的配列類の分析から、成熟鎖シード領域内では不安定さが低くなる傾向があることが示された(図9(h))。この理由から、この領域内にあるGC含有量を制限するために、miR−196a−2アルゴリズムに追加条件を組み込んだ。
下記の表4に実施例1−3で使用した配列類を示す(全て5’→3’方向)。
下記の表4に実施例1−3で使用した配列類を示す(全て5’→3’方向)。
<内在性miRNA類とmiR−196a−2スキャホールドとの適合性>
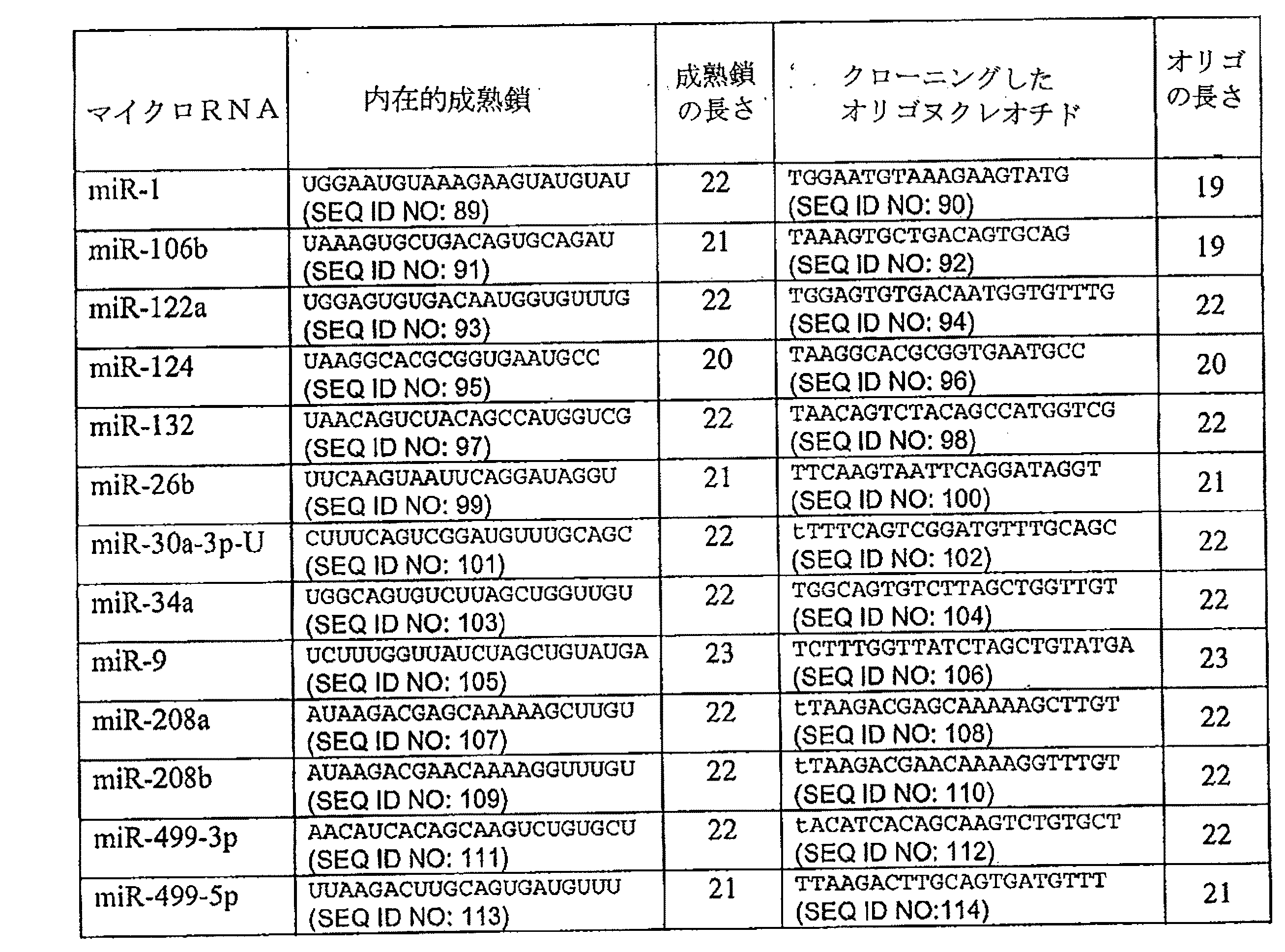
miR−196a−2スキャホールドを内在性miRNA類発現用の輸送プラットホームとして使用可能かどうかを決めるために、11個の別々の内在性成熟鎖配列類(miR−499−5p、miR−499−3p、−208a、−9、−34a、−30−3p、−132、−26b、−124、−208b、および122a)を、pG19SM6発現プラスミド内にあるmiR−196a−2スキャホールドにクローニングした。得られた構築体類は、第1のmiRNA由来のスキャホールドおよび第2のmiRNA由来の成熟鎖を含むようなshMIMICの例となる。この構築体類は次にあげる特徴をもつ。1)組み込まれた配列の長さは、19−23ヌクレオチド長であった。2)12位のミスマッチは保存された。3)成熟鎖1位のヌクレオチドは、常にUであった。もし、内在性miRNAの成熟鎖1位のヌクレオチドがUでない場合には、shMIMICではそのヌクレオチドをUに変換した。また、スキャホールドの2次構造を維持できる場合には、スター鎖上の5位、18位、19位、および21位にG:Uゆらぎ塩基対を形成させた。pG19SM6発現プラスミドにクローニングした配列類のリストを、表5に示す。ここで、成熟鎖1位が発現成熟鎖でUになるように修飾した位置を、下部にあるヌクレオチド類は示す。先に記載したように、発現ベクターに配列類をクローニングした。
miR−196a−2スキャホールドで機能する各miRNAの有効性を試験するために、特有の内在性miRNA配列を含む個々のmiR−196a−2発現カセットを、ヒト化Rluc遺伝子3’UTRに挿入したmiRを含有する2重ルシフェラーゼ構築体と並べて、先の実施例で記載した条件で細胞内にコットランスフェクションした。細胞を培養してFlucに対するRlucの比を測定した。
以上の研究結果から、細胞に内在性miRNA配列類を効率的に輸送するために、miR−196a−2スキャホールドを使用できることが明らかになった。図10に示すように、試験した構築体全てが、2重ルシフェラーゼレポーター構築体を70%以上サイレンシングした。これらの結果は、内在性miRNA輸送システムとしてmiR−196a−2スキャホールドが使用できることを示している。
また、挿入したmiRNAの長さを19個の塩基対で試験した実験も行った。例えば、22nt成熟鎖を3’末端で19ntに切り縮めてスキャホールドにクローニングした。表5に、クロ−ニングしたmiR−106bおよびmiR−1配列類を示す。全ての場合で、19ntに配列を切り縮めても各々のレポーター構築体をサイレンシングする能力に影響は無かった。従って、この結果から、miR−196a−2スキャホールドを、長さ19−23ntの外部miRNA配列類に適用できることが示される。また、miR−196a−2スキャホールドが11個の特有のmiRNA配列類を効果的に輸送できることから、ヒト、マウス、ラット、および、c.elegansを含む任意の種に由来するmiRNA類全てに、miR−196a−2スキャホールドを全般的に適用できることが示された。miR−196a−2スキャホールドに導入可能な成熟miRNA配列鎖類は、miRBase(http/microrna.sanger.ac.uk/sequences/)で見出すことができる。図11に、miR−196a−2スキャホールドに基づくshMIMIC用の一般的な設計思想を示す。
Claims (14)
- 幹−ループ構造をもつ核酸からなる非天然存在型miR−196a−2 miRNAであって、
前記幹−ループ構造の幹は成熟鎖−スター鎖2本鎖を組み込み、
前記成熟鎖の配列は、19から25個の塩基を有し、miR−196a−2の内在性成熟鎖の配列とは異なる配列であり、前記成熟鎖の2位から7位までは、標的RNAの一部に対し相補的であり、
前記成熟鎖の1位はUヌクレオチドであり、前記スター鎖は前記成熟鎖の1位に相対するヌクレオチドの位置にGヌクレオチドを有し、
前記2本鎖は、前記成熟鎖の12位にミスマッチを含むとともに(i)他にはミスマッチを含まない構成か、あるいは(ii)前記2本鎖の成熟鎖の5位、18位および19位の1以上の位置、及び20位から22位までの任意または全ての位置にミスマッチまたはゆらぎ塩基対を含む構成かのいずれかを有し、
前記2本鎖中その他の位置にはミスマッチまたはゆらぎ塩基対を含まない構成を有し、
前記成熟鎖の配列は5’位末端から符番されることを特徴とする非天然存在型miR−196a−2 miRNA。 - 請求項1に記載の非天然存在型miR−196a−2 miRNAであって、
内在性miR−196a−2の幹の配列からヌクレオチド1個を削除した配列、
内在性miR−196a−2の幹の配列にヌクレオチド1個を付加した配列、
内在性miR−196a−2の幹の配列でヌクレオチド1個を置換した配列、
内在性miR−196a−2のループの配列からヌクレオチド1個を削除した配列、
内在性miR−196a−2のループの配列にヌクレオチド1個を付加した配列、
内在性miR−196a−2のループの配列でヌクレオチド1個を置換した配列、
長さにおいて5個乃至150個の間のヌクレオチドをもつ5’フランキングヌクレオチド配列、および
長さにおいて5個乃至150個の間のヌクレオチドをもつ3’フランキングヌクレオチド配列の、少なくとも1つの配列を有する非天然存在型miR−196a−2 miRNA。 - 前記成熟鎖が、長さにおいて19個から23個の間のヌクレオチドからなることを特徴とする請求項1から請求項3のいずれか1項に記載の非天然存在型miR−196a−2 miRNA。
- 前記成熟鎖が、長さにおいて19個のヌクレオチドであることを特徴とする請求項1から請求項4のいずれか1項に記載の非天然存在型miR−196a−2 miRNA。
- 前記成熟鎖の配列がいかなる内在性miRNA成熟鎖とも異なることを特徴とする請求項1から請求項5のいずれか1項に記載の非天然存在型miR−196a−2 miRNA。
- 前記成熟鎖の配列がmiR−196a−2の内在性成熟鎖以外の内在性成熟miRNAから誘導されることを特徴とする請求項1から請求項5のいずれか1項に記載の非天然存在型miR−196a−2 miRNA。
- 請求項7に記載の非天然存在型miR−196a−2 miRNAであって、前記成熟鎖は、
hsa-let-7a-l, hsa-let-7a-2, hsa-let-7a-3, hsa-let-7b, hsa-let-7c, hsa-let-7d, hsa-let-7e, hsa-let-7f-l, hsa-let-7f-2, hsa-let-7g, hsa-let-7i, hsa-mir-1-1, hsa-mir-1-2, hsa-mir-7-1, hsa-mir-7-2, hsa-mir-7-3, hsa-mir-9-1, hsa-mir-9-2, hsa-mir-9-3, hsa-mir-10a, hsa-mir-10b, hsa-mir-15a, hsa-mir-15b, hsa-mir-16-1, hsa-mir-16-2, hsa-mir-17, hsa-mir-18a, hsa-mir-18b, hsa-mir-19a, hsa-mir-19b-l, hsa-mir-19b-2, hsa-mir-20a, hsa-mir-20b, hsa-mir-21, hsa-mir-22, hsa-mir-23a, hsa-mir-23b, hsa-mir-24-1, hsa-mir-24-2, hsa-mir-25, hsa-mir-26a-l, hsa-mir-26a-2, hsa-mir-26b, hsa-mir-27a, hsa-mir-27b, hsa-mir-28, hsa-mir-29a, hsa-mir-29b-l, hsa-mir-29b-2, hsa-mir-29c, hsa-mir-30a, hsa-mir-30b, hsa-mir-30c-l, hsa-mir-30c-2, hsa-mir-30d, hsa-mir-30e, hsa-mir-31, hsa-mir-32, hsa-mir-33a, hsa-mir-33b, hsa-mir-34a, hsa-mir-34b, hsa-mir-34c, hsa-mir-92a-l, hsa-mir-92a-2, hsa-mir-92-b, hsa-mir-93, hsa-mir-95, hsa-mir-96, hsa-mir-98, hsa-mir-99a, hsa-mir-99b, hsa-mir-100, hsa-mir-101-1, hsa-mir-101-2, hsa-mir-103-1, hsa-mir-103-2, hsa-mir-105-1, hsa-mir-105-2, hsa-mir-106a, hsa-mir-106b, hsa-mir-107, hsa-mir-122, hsa-mir-124-1, hsa-mir-124-2, hsa-mir-124-3, hsa-mir-125a, hsa-mir-125b-1, hsa-mir-125b-2, hsa-mir-126, hsa-mir-127, hsa-mir-128-1, hsa-mir-128-2, hsa-mir-129-1, hsa-mir-129-2, hsa-mir-130a, hsa-mir-130b, hsa-mir-132, hsa-mir-133a-l, hsa-mir-133a-2, hsa-mir-133b, hsa-mir-134, hsa-mir-135a-l, hsa-mir-135a-2, hsa-mir-135b, hsa-mir-136, hsa-mir-137, hsa-mir-138-1, hsa-mir-138-2, hsa-mir-139, hsa-mir-140, hsa-mir-141, hsa-mir-142, hsa-mir-143, hsa-mir-144, hsa-mir-145, hsa-mir-146a, hsa-mir-146b, hsa-mir-147, hsa-mir-147b, hsa-mir-148a, hsa-mir-148b, hsa-mir-149, hsa-mir-150, hsa-mir-151, hsa-mir-152, hsa-mir-153-1, hsa-mir-153-2, hsa-mir-154, hsa-mir-155, hsa-mir-181a-l, hsa-mir-181a-2, hsa-mir-181b-l, hsa-mir-18lb-2, hsa-mir-181c, hsa-mir-181d, hsa-mir-182, hsa-mir-183, hsa-mir-184, hsa-mir-185, hsa-mir-186, hsa-mir-187, hsa-mir-188, hsa-mir-190, hsa-mir-190b, hsa-mir-191, hsa-mir-192, hsa-mir-193a, hsa-mir-193b, hsa-mir-194-1, hsa-mir-194-2, hsa-mir-195, hsa-mir-196a-1, hsa-mir-196b, hsa-mir-197, hsa-mir-198, hsa-mir-199a-1, hsa-mir-199a-2, hsa-mir-199b, hsa-mir-200a, hsa-mir-200b, hsa-mir-200c, hsa-mir-202, hsa-mir-203, hsa-mir-204, hsa-mir-205, hsa-mir-206, hsa-mir-208a, hsa-mir-208b, hsa-mir-210, hsa-mir-211, hsa-mir-212, hsa-mir-214, hsa-mir-215, hsa-mir-216a, hsa-mir-216b, hsa-mir-217, hsa-mir-218-1, hsa-mir-218-2, hsa-mir-219-1, hsa-mir-219-2, hsa-mir-220a, hsa-mir-220b, hsa-mir-220c, hsa-mir-221, hsa-mir-222, hsa-mir-223, hsa-mir-224, hsa-mir-296, hsa-mir-297, hsa-mir-298, hsa-mir-299, hsa-mir-300, hsa-mir-301a, hsa-mir-301b, hsa-mir-302a, hsa-mir-302b, hsa-mir-302c, hsa-mir-302d, hsa-mir-302e, hsa-mir-302f, hsa-mir-320a, hsa-mir-320b-1, hsa-mir-320b-2, hsa-mir-320c-1, hsa-mir-320c-2, hsa-mir-320d-l, hsa-mir-320d-2, hsa-mir-323, hsa-mir-324, hsa-mir-325, hsa-mir-326, hsa-mir-328, hsa-mir-329-1, hsa-mir-329-2, hsa-mir-330, hsa-mir-331, hsa-mir-335, hsa-mir-337, hsa-mir-338, hsa-mir-339, hsa-mir-340, hsa-mir-342, hsa-mir-345, hsa-mir-346, hsa-mir-361, hsa-mir-362, hsa-mir-363, hsa-mir-365-1, hsa-mir-365-2, hsa-mir-367, hsa-mir-369, hsa-mir-370, hsa-mir-371, hsa-mir-372, hsa-mir-373, hsa-mir-374a, hsa-mir-374b, hsa-mir-375, hsa-mir-376a-l, hsa-mir-376a-2, hsa-mir-376b, hsa-mir-376c, hsa-mir-377, hsa-mir-378, hsa-mir-379, hsa-mir-380, hsa-mir-381, hsa-mir-382, hsa-mir-383, hsa-mir-384, hsa-mir-409, hsa-mir-410, hsa-mir-411, hsa-mir-412, hsa-mir-421, hsa-mir-422a, hsa-mir-423, hsa-mir-424, hsa-mir-425, hsa-mir-429, hsa-mir-431, hsa-mir-432, hsa-mir-433, hsa-mir-448, hsa-mir-449a, hsa-mir-449b, hsa-mir-450a-l, hsa-mir-450a-2, hsa-mir-450b, hsa-mir-451, hsa-mir-452, hsa-mir-453, hsa-mir-454, hsa-mir-455, hsa-mir-483, hsa-mir-484, hsa-mir-485, hsa-mir-486, hsa-mir-487a, hsa-mir-487b, hsa-mir-488, hsa-mir-489, hsa-mir-490, hsa-mir-491, hsa-mir-492, hsa-mir-493, hsa-mir-494, hsa-mir-495, hsa-mir-496, hsa-mir-497, hsa-mir-498, hsa-mir-499, hsa-mir-500, hsa-mir-501, hsa-mir-502, hsa-mir-503, hsa-mir-504, hsa-mir-505, hsa-mir-506, hsa-mir-507, hsa-mir-508, hsa-mir-509-1, hsa-mir-509-2, hsa-mir-509-3, hsa-mir-510, hsa-mir-511-1, hsa-mir-511-2, hsa-mir-512-1, hsa-mir-512-2, hsa-mir-513a-l, hsa-mir-513a-2, hsa-mir-513b, hsa-mir-513c, hsa-mir-514-1, hsa-mir-514-2, hsa-mir-514-3, hsa-mir-515-1, hsa-mir-515-2, hsa-mir-516a-l, hsa-mir-516a-2, hsa-mir-516b-l, hsa-mir-516b-2, hsa-mir-517a, hsa-mir-517b, hsa-mir-517c, hsa-mir-518a-l, hsa-mir-518a-2, hsa-mir-518b, hsa-mir-518c, hsa-mir-518d, hsa-mir-518e, hsa-mir-518f, hsa-mir-519a-l, hsa-mir-519a-2, hsa-mir-519b, hsa-mir-519c, hsa-mir-519d, hsa-mir-519e, hsa-mir-520a, hsa-mir-520b, hsa-mir-520c, hsa-mir-520d, hsa-mir-520e, hsa-mir-520f, hsa-mir-520g, hsa-mir-520h, hsa-mir-521-1, hsa-mir-521-2, hsa-mir-522, hsa-mir-523, hsa-mir-524, hsa-mir-525, hsa-mir-526a-l, hsa-mir-526a-2, hsa-mir-526b, hsa-mir-527, hsa-mir-532, hsa-mir-539, hsa-mir-541, hsa-mir-542, hsa-mir-543, hsa-mir-544, hsa-mir-545, hsa-mir-548a-l, hsa-mir-548a-2, hsa-mir-548a-3, hsa-mir-548b, hsa-mir-548c, hsa-mir-548d-l, hsa-mir-548d-2, hsa-mir-548e, hsa-mir-548f-l, hsa-mir-548f-2, hsa-mir-548f-3, hsa-mir-548f-4, hsa-mir-548f-5, hsa-mir-548g, hsa-mir-548h-l, hsa-mir-548h-2, hsa-mir-548h-3, hsa-mir-548h-4, hsa-mir-548i-l, hsa-mir-548i-2, hsa-mir-548i-3, hsa-mir-548i-4, hsa-mir-548j, hsa-mir-548k, hsa-mir-548l, hsa-mir-548m, hsa-mir-548n, hsa-mir-548o, hsa-mir-548p, hsa-mir-549, hsa-mir-550-1, hsa-mir-550-2, hsa-mir-551a, hsa-mir-551b, hsa-mir-552, hsa-mir-553, hsa-mir-554, hsa-mir-555, hsa-mir-556, hsa-mir-557, hsa-mir-558, hsa-mir-559, hsa-mir-561, hsa-mir-562, hsa-mir-563, hsa-mir-564, hsa-mir-566, hsa-mir-567, hsa-mir-568, hsa-mir-569, hsa-mir-570, hsa-mir-571, hsa-mir-572, hsa-mir-573, hsa-mir-574, hsa-mir-575, hsa-mir-576, hsa-mir-577, hsa-mir-578, hsa-mir-579, hsa-mir-580, hsa-mir-581, hsa-mir-582, hsa-mir-583, hsa-mir-584, hsa-mir-585, hsa-mir-586, hsa-mir-587, hsa-mir-588, hsa-mir-589, hsa-mir-590, hsa-mir-591, hsa-mir-592, hsa-mir-593, hsa-mir-595, hsa-mir-596, hsa-mir-597, hsa-mir-598, hsa-mir-599, hsa-mir-600, hsa-mir-601, hsa-mir-602, hsa-mir-603, hsa-mir-604, hsa-mir-605, hsa-mir-606, hsa-mir-607, hsa-mir-608, hsa-mir-609, hsa-mir-610, hsa-mir-611, hsa-mir-612, hsa-mir-613, hsa-mir-614, hsa-mir-615, hsa-mir-616, hsa-mir-617, hsa-mir-618, hsa-mir-619, hsa-mir-620, hsa-mir-621, hsa-mir-622, hsa-mir-623, hsa-mir-624, hsa-mir-625, hsa-mir-626, hsa-mir-627, hsa-mir-628, hsa-mir-629, hsa-mir-630, hsa-mir-631, hsa-mir-632, hsa-mir-633, hsa-mir-634, hsa-mir-635, hsa-mir-636, hsa-mir-637, hsa-mir-638, hsa-mir-639, hsa-mir-640, hsa-mir-641, hsa-mir-642, hsa-mir-643, hsa-mir-644, hsa-mir-645, hsa-mir-646, hsa-mir-647, hsa-mir-648, hsa-mir-649, hsa-mir-650, hsa-mir-651, hsa-mir-652, hsa-mir-653, hsa-mir-654, hsa-mir-655, hsa-mir-656, hsa-mir-657, hsa-mir-658, hsa-mir-659, hsa-mir-660, hsa-mir-661, hsa-mir-662, hsa-mir-663, hsa-mir-663b, hsa-mir-664, hsa-mir-665, hsa-mir-668, hsa-mir-671, hsa-mir-675, hsa-mir-708, hsa-mir-720, hsa-mir-744, hsa-mir-758, hsa-mir-760, hsa-mir-765, hsa-mir-766, hsa-mir-767, hsa-mir-768, hsa-mir-769, hsa-mir-770, hsa-mir-802, hsa-mir-873, hsa-mir-874, hsa-mir-875, hsa-mir-876, hsa-mir-877, hsa-mir-885, hsa-mir-886, hsa-mir-887, hsa-mir-888, hsa-mir-889, hsa-mir-890, hsa-mir-891a, hsa-mir-891b, hsa-mir-892a, hsa-mir-892b, hsa-mir-920, hsa-mir-921, hsa-mir-922, hsa-mir-923, hsa-mir-924, hsa-mir-933, hsa-mir-934, hsa-mir-935, hsa-mir-936, hsa-mir-937, hsa-mir-938, hsa-mir-939, hsa-mir-940, hsa-mir-941-1, hsa-mir-941-2, hsa-mir-941-3, hsa-mir-941-4, hsa-mir-942, hsa-mir-943, hsa-mir-944, hsa-mir-1178, hsa-mir-1179, hsa-mir-1180, hsa-mir-1181, hsa-mir-1182, hsa-mir-1183, hsa-mir-1184, hsa-mir-1185-1, hsa-mir-1185-2, hsa-mir-1197, hsa-mir-1200, hsa-mir-1201, hsa-mir-1202, hsa-mir-1203, hsa-mir-1204, hsa-mir-1205, hsa-mir-1206, hsa-mir-1207, hsa-mir-1208, hsa-mir-1224, hsa-mir-1225, hsa-mir-1226, hsa-mir-1227, hsa-mir-1228, hsa-mir-1229, hsa-mir-1231, hsa-mir-1233, hsa-mir-1234, hsa-mir-1236, hsa-mir-1237, hsa-mir-1238, hsa-mir-1243, hsa-mir-1244, hsa-mir-1245, hsa-mir-1246, hsa-mir-1247, hsa-mir-1248, hsa-mir-1249, hsa-mir-1250, hsa-mir-1251, hsa-mir-1252, hsa-mir-1253, hsa-mir-1254, hsa-mir-1255a, hsa-mir-1255b-1, hsa-mir-1255b-2, hsa-mir-1256, hsa-mir-1257, hsa-mir-1258, hsa-mir-1259, hsa-mir-1260, hsa-mir-1261, hsa-mir-1262, hsa-mir-1263, hsa-mir-1264, hsa-mir-1265, hsa-mir-1266, hsa-mir-1267, hsa-mir-1268, hsa-mir-1269, hsa-mir-1270, hsa-mir-1271, hsa-mir-1272, hsa-mir-1273, hsa-mir-1274a, hsa-mir-1274b, hsa-mir-1275, hsa-mir-1276, hsa-mir-1277, hsa-mir-1278, hsa-mir-1279, hsa-mir-1280, hsa-mir-1281, hsa-mir-1282, hsa-mir-1283-1, hsa-mir-1283-2, hsa-mir-1284, hsa-mir-1285-1, hsa-mir-1285-2, hsa-mir-1286, hsa-mir-1287, hsa-mir-1288, hsa-mir-1289-1, hsa-mir-1289-2, hsa-mir-1290, hsa-mir-1291, hsa-mir-1292, hsa-mir-1293, hsa-mir-1294, hsa-mir-1295, hsa-mir-1296, hsa-mir-1297, hsa-mir-1298, hsa-mir-1299, hsa-mir-1300, hsa-mir-1301, hsa-mir-1302-1, hsa-mir-1302-2, hsa-mir-1302-3, hsa-mir-1302-4, hsa-mir-1302-5, hsa-mir-1302-6, hsa-mir-1302-7, hsa-mir-1302-8, hsa-mir-1303, hsa-mir-1304, hsa-mir-1305, hsa-mir-1306, hsa-mir-1307, hsa-mir-1308, hsa-mir-1321, hsa-mir-1322, hsa-mir-1323, hsa-mir-1324, hsa-mir-1825, hsa-mir-1826, hsa-mir-1827
から構成される群から選択されるmiRNAの内在性成熟鎖配列から誘導されることを特徴とする非天然存在型miR−196a−2 miRNA。 - 請求項1から請求項8のいずれか1項に記載の非天然存在型miRNAをコードするヌクレオチド配列を有するリコンビナント発現ベクター。
- 前記ベクターは人工イントロンを有するレポーター遺伝子と操作によって結合しているプロモーターを有し、および前記人工イントロン内部に前記非天然存在型miRNAが位置することを特徴とする請求項9に記載のリコンビナント発現ベクター。
- 前記ベクターは3’非翻訳領域(UTR)をもつレポーター遺伝子と操作によって結合しているプロモーターを有し、および前記3’UTR内部に前記非天然存在型miRNAが位置することを特徴とする請求項9に記載のリコンビナント発現ベクター。
- 前記ベクターはレンチウイルスベクターであることを特徴とする請求項9から請求項11のいずれか1項に記載のリコンビナント発現ベクター。
- 請求項1から請求項8のいずれか1項に記載の非天然存在型miRNAまたは請求項9から請求項12のいずれか1項に記載のリコンビナント発現ベクターを有し、さらに薬学的に許容されるキャリアーを少なくとも1つ有する医薬品組成物。
- インビトロの細胞内標的RNAの機能を低下させる方法であって、前記方法は、
前記細胞を、請求項1から請求項8のいずれか1項に記載の非天然存在型miRNAまたは請求項9から請求項12のいずれか1項に記載のリコンビナント発現ベクターに接触させる工程を有し、前記非天然存在型miRNAは前記細胞内で処理されて前記成熟鎖の配列をもつ成熟miRNAを生成することを特徴とする、細胞内標的RNAの機能を低下させる方法。
Applications Claiming Priority (2)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| US93978507P | 2007-05-23 | 2007-05-23 | |
| US60/939,785 | 2007-05-23 |
Related Parent Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2010509546A Division JP5637533B2 (ja) | 2007-05-23 | 2008-05-22 | マイクロ−rnaスキャホールドおよび非天然存在型マイクロ−rna |
Publications (1)
| Publication Number | Publication Date |
|---|---|
| JP2014207909A true JP2014207909A (ja) | 2014-11-06 |
Family
ID=40075484
Family Applications (2)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2010509546A Active JP5637533B2 (ja) | 2007-05-23 | 2008-05-22 | マイクロ−rnaスキャホールドおよび非天然存在型マイクロ−rna |
| JP2014116024A Pending JP2014207909A (ja) | 2007-05-23 | 2014-06-04 | マイクロ−rnaスキャホールドおよび非天然存在型マイクロ−rna |
Family Applications Before (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2010509546A Active JP5637533B2 (ja) | 2007-05-23 | 2008-05-22 | マイクロ−rnaスキャホールドおよび非天然存在型マイクロ−rna |
Country Status (6)
| Country | Link |
|---|---|
| US (4) | US8841267B2 (ja) |
| EP (2) | EP2155911B1 (ja) |
| JP (2) | JP5637533B2 (ja) |
| AU (1) | AU2008256886B2 (ja) |
| CA (1) | CA2687336C (ja) |
| WO (2) | WO2008147837A1 (ja) |
Families Citing this family (52)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| US8592384B2 (en) | 2005-04-04 | 2013-11-26 | The Board Of Regents Of The University Of Texas System | Micro-RNA's that regulate muscle cells |
| MX2009001281A (es) | 2006-08-01 | 2009-04-16 | Univ Texas | Identificacion de un micro-arn que activa la expresion de la cadena pesada de beta-miosina. |
| JP5637533B2 (ja) | 2007-05-23 | 2014-12-10 | ジーイー ヘルスケア ダーマコン,インク. | マイクロ−rnaスキャホールドおよび非天然存在型マイクロ−rna |
| US8841437B2 (en) * | 2008-06-20 | 2014-09-23 | The Board Of Trustees Of The Leland Stanford Junior University | Precursor miRNA loop-modulated target regulation |
| KR20100057022A (ko) | 2007-07-31 | 2010-05-28 | 보드 오브 리전츠 더 유니버시티 오브 텍사스 시스템 | 마이오신 발현 및 근섬유 동일성을 제어하는 마이크로-rnas |
| ES2621161T3 (es) | 2007-07-31 | 2017-07-03 | The Board Of Regents Of The University Of Texas System | Familia de micro-ARN que modula la fibrosis y usos de la misma |
| KR20100099158A (ko) | 2007-11-09 | 2010-09-10 | 보드 오브 리전츠 더 유니버시티 오브 텍사스 시스템 | 심근세포 생존과 심장 회복을 제어하는 MIR-15 집단의 마이크로RNAs |
| CN102036689B (zh) | 2008-03-17 | 2014-08-06 | 得克萨斯系统大学董事会 | 神经肌肉突触维持和再生中涉及的微小rna的鉴定 |
| US9217155B2 (en) | 2008-05-28 | 2015-12-22 | University Of Massachusetts | Isolation of novel AAV'S and uses thereof |
| BRPI1008517A2 (pt) | 2009-02-04 | 2016-03-08 | Univ Texas | direcionamento duplo de mir-208 e mir-499 no tratamento de doenças cardíacas. |
| US8734809B2 (en) | 2009-05-28 | 2014-05-27 | University Of Massachusetts | AAV's and uses thereof |
| JP2011004708A (ja) * | 2009-06-29 | 2011-01-13 | Univ Of Tokyo | smallRNA二本鎖およびヘアピン型RNAの設計方法 |
| WO2011133901A2 (en) | 2010-04-23 | 2011-10-27 | University Of Massachusetts | Aav-based treatment of cholesterol-related disorders |
| DK2826860T3 (en) | 2010-04-23 | 2018-12-03 | Univ Massachusetts | CNS targeting AAV vectors and methods for their use |
| WO2011133874A1 (en) | 2010-04-23 | 2011-10-27 | University Of Massachusetts | Multicistronic expression constructs |
| RU2585491C2 (ru) | 2010-06-04 | 2016-05-27 | Борд Оф Риджентс, Зе Юниверсити Оф Техас Систем | Регуляция метаболизма с помощью mir-378 |
| SG190355A1 (en) | 2010-12-15 | 2013-07-31 | Miragen Therapeutics | Microrna inhibitors comprising locked nucleotides |
| EP3318635A1 (en) | 2011-04-21 | 2018-05-09 | University of Massachusetts | Raav-based compositions and methods for treating alpha-1 anti-trypsin deficiencies |
| EP2717883B1 (en) | 2011-05-02 | 2017-03-22 | Stichting VUmc | Protection against endothelial barrier dysfunction through inhibition of the tyrosine kinase abl-related gene (arg) |
| WO2013003350A2 (en) * | 2011-06-27 | 2013-01-03 | Eisai R&D Management Co., Ltd. | Microrna biomarkers indicative of alzheimer's disease |
| US9481895B2 (en) | 2011-09-23 | 2016-11-01 | Ge Healthcare Dharmacon, Inc. | Introduction of modular vector elements during production of a lentivirus |
| EP2764123B1 (en) * | 2011-10-05 | 2019-01-16 | Dharmacon, Inc. | Optimization of vectors for effective delivery and expression of genetic content |
| US9428749B2 (en) | 2011-10-06 | 2016-08-30 | The Board Of Regents, The University Of Texas System | Control of whole body energy homeostasis by microRNA regulation |
| US9334498B2 (en) | 2012-05-10 | 2016-05-10 | Uab Research Foundation | Methods and compositions for modulating MIR-204 activity |
| WO2013180038A1 (ja) | 2012-05-26 | 2013-12-05 | 株式会社ボナック | デリバリー機能を有する遺伝子発現制御用の一本鎖核酸分子 |
| US9388408B2 (en) | 2012-06-21 | 2016-07-12 | MiRagen Therapeutics, Inc. | Oligonucleotide-based inhibitors comprising locked nucleic acid motif |
| US9163235B2 (en) | 2012-06-21 | 2015-10-20 | MiRagen Therapeutics, Inc. | Inhibitors of the miR-15 family of micro-RNAs |
| WO2014171826A1 (en) | 2013-04-17 | 2014-10-23 | Stichting Vu-Vumc | Treatment of cognitive impairment in depressive disorders |
| CN105899663B (zh) * | 2013-12-26 | 2019-07-26 | 学校法人东京医科大学 | 用于基因表达控制的人工模拟miRNA及其用途 |
| CN106068324B (zh) | 2013-12-27 | 2020-12-29 | 株式会社博纳克 | 控制基因表达的人工匹配型miRNA及其用途 |
| WO2015112837A1 (en) * | 2014-01-24 | 2015-07-30 | Georgetown University | Biomarkers and therapeutic targets for abnormal retinal pigment epithelium |
| US10072251B2 (en) | 2014-02-19 | 2018-09-11 | University Of Massachusetts | Recombinant AAVS having useful transcytosis properties |
| EP3750907A3 (en) | 2014-03-18 | 2021-04-28 | University of Massachusetts | Raav-based compositions and methods for treating amyotrophic lateral sclerosis |
| US10975391B2 (en) | 2014-04-25 | 2021-04-13 | University Of Massachusetts | Recombinant AAV vectors useful for reducing immunity against transgene products |
| EP3160980B1 (en) | 2014-05-28 | 2020-05-20 | The Regents of the University of California | HYBRID tRNA/pre-miRNA MOLECULES AND METHODS OF USE |
| WO2016054554A1 (en) | 2014-10-03 | 2016-04-07 | University Of Massachusetts | Heterologous targeting peptide grafted aavs |
| CN107073051B (zh) | 2014-10-21 | 2021-08-24 | 马萨诸塞大学 | 重组aav变体及其用途 |
| MX2017008587A (es) | 2014-12-27 | 2017-10-20 | Bonac Corp | Mirna natural para controlar la expresion de gen y uso del mismo. |
| KR20170103841A (ko) | 2015-01-20 | 2017-09-13 | 미라젠 세러퓨틱스 인코포레이티드 | Mir-92 억제제 및 이의 용도 |
| EP3256170B1 (en) | 2015-02-13 | 2020-09-23 | University of Massachusetts | Compositions and methods for transient delivery of nucleases |
| JP6602847B2 (ja) | 2015-03-27 | 2019-11-06 | 株式会社ボナック | デリバリー機能と遺伝子発現制御能を有する一本鎖核酸分子 |
| US11046955B2 (en) | 2015-04-24 | 2021-06-29 | University Of Massachusetts | Modified AAV constructs and uses thereof |
| CA3012344A1 (en) | 2016-02-12 | 2017-08-17 | University Of Massachusetts | Anti-angiogenic mirna therapeutics for inhibiting corneal neovascularization |
| US10457940B2 (en) | 2016-09-22 | 2019-10-29 | University Of Massachusetts | AAV treatment of Huntington's disease |
| US11578340B2 (en) | 2016-10-13 | 2023-02-14 | University Of Massachusetts | AAV capsid designs |
| WO2018111099A1 (en) | 2016-12-12 | 2018-06-21 | Stichting Vumc | Biomarkers and treatments for cerebral amyloid angiopathy (caa) |
| WO2018208972A1 (en) | 2017-05-09 | 2018-11-15 | University Of Massachusetts | Methods of treating amyotrophic lateral sclerosis (als) |
| WO2019060686A1 (en) | 2017-09-22 | 2019-03-28 | University Of Massachusetts | NEW DUAL EXPRESSION VECTORS OF SOD1 AND USES THEREOF |
| WO2020067887A1 (en) | 2018-09-24 | 2020-04-02 | Erasmus University Medical Center Rotterdam | Specific inhibition of janus kinase 3 (jak3) for modulating anti-tumor immune responses |
| KR20220035326A (ko) | 2019-05-02 | 2022-03-22 | 셀리아드 | 다중화된 억제성 rna를 갖는 세포 |
| CN114144202A (zh) * | 2019-05-02 | 2022-03-04 | 达尔马科恩有限公司 | 用于载体的多重shRNA |
| GB202112471D0 (en) * | 2021-09-01 | 2021-10-13 | King S College London | Microna systems |
Citations (1)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| JP5637533B2 (ja) * | 2007-05-23 | 2014-12-10 | ジーイー ヘルスケア ダーマコン,インク. | マイクロ−rnaスキャホールドおよび非天然存在型マイクロ−rna |
Family Cites Families (9)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| US20060217331A1 (en) | 2001-05-18 | 2006-09-28 | Sirna Therapeutics, Inc. | Chemically modified double stranded nucleic acid molecules that mediate RNA interference |
| US7892793B2 (en) * | 2002-11-04 | 2011-02-22 | University Of Massachusetts | Allele-specific RNA interference |
| EP2314691A3 (en) * | 2002-11-14 | 2012-01-18 | Dharmacon, Inc. | Fuctional and hyperfunctional siRNA |
| JP2006519008A (ja) | 2003-02-10 | 2006-08-24 | 独立行政法人産業技術総合研究所 | 哺乳動物細胞の調節 |
| US8106180B2 (en) * | 2003-08-07 | 2012-01-31 | Whitehead Institute For Biomedical Research | Methods and products for expression of micro RNAs |
| EP2471924A1 (en) * | 2004-05-28 | 2012-07-04 | Asuragen, INC. | Methods and compositions involving microRNA |
| US20060200878A1 (en) * | 2004-12-21 | 2006-09-07 | Linda Lutfiyya | Recombinant DNA constructs and methods for controlling gene expression |
| US20060185027A1 (en) | 2004-12-23 | 2006-08-17 | David Bartel | Systems and methods for identifying miRNA targets and for altering miRNA and target expression |
| EP1896587A2 (en) * | 2005-05-31 | 2008-03-12 | Cold Spring Harbor Laboratory | METHODS FOR PRODUCING MICRORNAs |
-
2008
- 2008-05-22 JP JP2010509546A patent/JP5637533B2/ja active Active
- 2008-05-22 EP EP08780685.7A patent/EP2155911B1/en active Active
- 2008-05-22 US US12/601,506 patent/US8841267B2/en active Active
- 2008-05-22 CA CA2687336A patent/CA2687336C/en active Active
- 2008-05-22 US US12/601,508 patent/US9353368B2/en active Active
- 2008-05-22 AU AU2008256886A patent/AU2008256886B2/en active Active
- 2008-05-22 EP EP08769579.7A patent/EP2160477B1/en active Active
- 2008-05-22 WO PCT/US2008/064458 patent/WO2008147837A1/en active Application Filing
- 2008-05-22 WO PCT/US2008/064462 patent/WO2008147839A1/en active Application Filing
-
2014
- 2014-06-04 JP JP2014116024A patent/JP2014207909A/ja active Pending
- 2014-07-30 US US14/447,359 patent/US9284554B2/en active Active
- 2014-08-07 US US14/454,436 patent/US20140343130A1/en not_active Abandoned
Patent Citations (1)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| JP5637533B2 (ja) * | 2007-05-23 | 2014-12-10 | ジーイー ヘルスケア ダーマコン,インク. | マイクロ−rnaスキャホールドおよび非天然存在型マイクロ−rna |
Also Published As
| Publication number | Publication date |
|---|---|
| US20100292310A1 (en) | 2010-11-18 |
| CA2687336A1 (en) | 2008-12-04 |
| AU2008256886B2 (en) | 2013-02-28 |
| AU2008256886A1 (en) | 2008-12-04 |
| EP2160477A1 (en) | 2010-03-10 |
| CA2687336C (en) | 2014-12-23 |
| EP2155911B1 (en) | 2013-08-28 |
| EP2160477B1 (en) | 2013-08-07 |
| US20140343130A1 (en) | 2014-11-20 |
| US9353368B2 (en) | 2016-05-31 |
| WO2008147839A1 (en) | 2008-12-04 |
| EP2155911A1 (en) | 2010-02-24 |
| US8841267B2 (en) | 2014-09-23 |
| WO2008147837A1 (en) | 2008-12-04 |
| JP2010527616A (ja) | 2010-08-19 |
| US9284554B2 (en) | 2016-03-15 |
| US20140336242A1 (en) | 2014-11-13 |
| US20100256222A1 (en) | 2010-10-07 |
| EP2160477A4 (en) | 2011-10-26 |
| JP5637533B2 (ja) | 2014-12-10 |
| EP2155911A4 (en) | 2011-10-26 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| JP5637533B2 (ja) | マイクロ−rnaスキャホールドおよび非天然存在型マイクロ−rna | |
| US10612026B2 (en) | Pharmaceutical composition for treating cancer comprising microrna as active ingredient | |
| AU2007323469B2 (en) | Oligonucleotides for modulating target RNA activity | |
| EP2550360B1 (en) | Bivalent antisense oligonucleotides | |
| US20140080894A1 (en) | Enhanced biodistribution of oligomers | |
| US11602568B2 (en) | Engineered B lymphocytes and compositions having micro-RNA and methods for making and using them | |
| US11041201B2 (en) | Methods for detection of RNase activity | |
| CN101641440A (zh) | 用于调节靶rna活性的寡核苷酸 | |
| AU2014250708B2 (en) | Oligonucleotides for modulating target RNA activity |
Legal Events
| Date | Code | Title | Description |
|---|---|---|---|
| A711 | Notification of change in applicant |
Free format text: JAPANESE INTERMEDIATE CODE: A711 Effective date: 20150227 |
|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A821 Effective date: 20150227 |
|
| A131 | Notification of reasons for refusal |
Free format text: JAPANESE INTERMEDIATE CODE: A132 Effective date: 20150818 |
|
| A02 | Decision of refusal |
Free format text: JAPANESE INTERMEDIATE CODE: A02 Effective date: 20160510 |