KR20230038503A - 샤르코-마리-투스 질환의 치료에 유용한 조성물 - Google Patents
샤르코-마리-투스 질환의 치료에 유용한 조성물 Download PDFInfo
- Publication number
- KR20230038503A KR20230038503A KR1020237003861A KR20237003861A KR20230038503A KR 20230038503 A KR20230038503 A KR 20230038503A KR 1020237003861 A KR1020237003861 A KR 1020237003861A KR 20237003861 A KR20237003861 A KR 20237003861A KR 20230038503 A KR20230038503 A KR 20230038503A
- Authority
- KR
- South Korea
- Prior art keywords
- seq
- leu
- sequence
- mirna
- val
- Prior art date
Links
Images
Classifications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/63—Introduction of foreign genetic material using vectors; Vectors; Use of hosts therefor; Regulation of expression
- C12N15/79—Vectors or expression systems specially adapted for eukaryotic hosts
- C12N15/85—Vectors or expression systems specially adapted for eukaryotic hosts for animal cells
- C12N15/86—Viral vectors
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K45/00—Medicinal preparations containing active ingredients not provided for in groups A61K31/00 - A61K41/00
- A61K45/06—Mixtures of active ingredients without chemical characterisation, e.g. antiphlogistics and cardiaca
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K48/00—Medicinal preparations containing genetic material which is inserted into cells of the living body to treat genetic diseases; Gene therapy
- A61K48/005—Medicinal preparations containing genetic material which is inserted into cells of the living body to treat genetic diseases; Gene therapy characterised by an aspect of the 'active' part of the composition delivered, i.e. the nucleic acid delivered
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61P—SPECIFIC THERAPEUTIC ACTIVITY OF CHEMICAL COMPOUNDS OR MEDICINAL PREPARATIONS
- A61P25/00—Drugs for disorders of the nervous system
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K14/00—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof
- C07K14/435—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof from animals; from humans
- C07K14/46—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof from animals; from humans from vertebrates
- C07K14/47—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof from animals; from humans from vertebrates from mammals
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/11—DNA or RNA fragments; Modified forms thereof; Non-coding nucleic acids having a biological activity
- C12N15/113—Non-coding nucleic acids modulating the expression of genes, e.g. antisense oligonucleotides; Antisense DNA or RNA; Triplex- forming oligonucleotides; Catalytic nucleic acids, e.g. ribozymes; Nucleic acids used in co-suppression or gene silencing
- C12N15/1137—Non-coding nucleic acids modulating the expression of genes, e.g. antisense oligonucleotides; Antisense DNA or RNA; Triplex- forming oligonucleotides; Catalytic nucleic acids, e.g. ribozymes; Nucleic acids used in co-suppression or gene silencing against enzymes
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N9/00—Enzymes; Proenzymes; Compositions thereof; Processes for preparing, activating, inhibiting, separating or purifying enzymes
- C12N9/14—Hydrolases (3)
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Y—ENZYMES
- C12Y306/00—Hydrolases acting on acid anhydrides (3.6)
- C12Y306/05—Hydrolases acting on acid anhydrides (3.6) acting on GTP; involved in cellular and subcellular movement (3.6.5)
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K2300/00—Mixtures or combinations of active ingredients, wherein at least one active ingredient is fully defined in groups A61K31/00 - A61K41/00
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2310/00—Structure or type of the nucleic acid
- C12N2310/10—Type of nucleic acid
- C12N2310/12—Type of nucleic acid catalytic nucleic acids, e.g. ribozymes
- C12N2310/122—Hairpin
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2310/00—Structure or type of the nucleic acid
- C12N2310/10—Type of nucleic acid
- C12N2310/14—Type of nucleic acid interfering N.A.
- C12N2310/141—MicroRNAs, miRNAs
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2750/00—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA ssDNA viruses
- C12N2750/00011—Details
- C12N2750/14011—Parvoviridae
- C12N2750/14111—Dependovirus, e.g. adenoassociated viruses
- C12N2750/14141—Use of virus, viral particle or viral elements as a vector
- C12N2750/14143—Use of virus, viral particle or viral elements as a vector viral genome or elements thereof as genetic vector
Abstract
하기를 포함하는 CMT2를 갖는 환자를 치료하는데 유용한 rAAV 및 다른 벡터 및 조성물이 본원에 제공된다: (a) 조작된 인간 미토푸신 2 암호화 서열을 암호화하는 재조합 핵산 서열로서, 조작된 인간 미토푸신 2 암호화 서열이 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되는, 재조합 핵산 서열. 또한, 하기를 포함하는 CMT2를 갖는 환자를 치료하는데 유용한 rAAV 및 다른 벡터 및 조성물이 제공된다: (b) 인간 CMT2A 대상체에서 내인성 인간 미토푸신 2 서열에 특이적인 적어도 하나의 miRNA를 암호화하는 핵산 서열로서, 상기 miRNA 암호화 서열은 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되는, 핵산 서열. 조작된 hMfn2 암호화 서열 및 적어도 하나의 miRNA 암호화 서열을 모두 함유하는 조성물로서, 상기 조작된 인간 미토푸신 2 암호화 서열은 암호화된 miRNA의 표적 부위에서 CMT2A 환자의 내인성 인간 미토푸신 2와 상이한 서열을 갖는, 조성물이 추가로 제공된다.
Description
샤르코-마리-투스(CMT) 신경병증은 말초 신경에서 발견되는 이질적인 유전성 질환군이다. CMT는 어린이와 성인 모두에게 영향을 미치는 일반적인 장애이다. 샤르코-마리 투스 질환(CMT) 또는 유전성 운동 및 감각 신경병증(HMSN)은 증후군의 일부가 아닌 유전성 신경병증에 가장 일반적으로 사용되는 명칭이다(Klein, C. J., Duan, X., Shy, M. E., 2013. Inherited neuropathies: Clinical overview and update. Muscle Nerve; Bassam, B., 2014. Charcot-Marie-Tooth Disease Variants- Classification, Clinical, and Genetic Features and Rational Diagnostic Evaluation. J. Clin. Neuromusc. Dis. 15, 117-128; Scherer, S. S., Shy, M. E., 2015. CMT Subtypes and Disease Burden in Patients Enrolled in the INC Natural History Study (6601) from 2009-2013. J. Neurol. Neurosurg. Psychiat. 86, 873-878).
우세하게 유전되는 CMT 신경병증(제2형 CMT 장애)의 축삭 형태는 감소된 운동 및 감각 복합 활동 전위 진폭과 더불어 정상 또는 약간 감소된 속도를 가지며, 축삭 손실은 생검된 신경에서 주요 소견이다. 미토콘드리아 융합 및 축삭을 따라 수송에 필요한 단백질인, 미토푸신2(MFN2) 유전자의 우성 돌연변이가 CMT2A를 유발한다(Zuchner, S. 등, 2004. Mutations in the mitochondrial GTPase mitofusin 2 cause Charcot-Marie-Tooth neuropathy type 2A. Nat Genet 36, 449-451). CMT2A는 전체 CMT의 최대 7%를 유발하는 것으로 추정되며, 제2형 CMT의 가장 일반적인 형태이다(Freidman, V. 등, 2015. CMT Subtypes and Disease Burden in Patients Enrolled in the INC Natural History Study (6601) from 2009-2013. J. Neurol. Neurosurg. Psychiat. 86, 873-878). 상이한 MFN2 돌연변이는 상이한 정도의 신경병증을 유발한다.
대부분의 MFN2 돌연변이는 중증의 조기 발병 축삭 신경병증을 유발하며, 드 노보(de novo) 돌연변이이다. 다른 MFN2 우성 돌연변이는 나중에 발병함에 따라 더 경미한 축삭 신경병증을 유발한다(Lawson, V. H. 등, 2005. Clinical and electrophysiologic features of CMT2A with mutations in the mitofusin 2 gene. Neurology 65, 197-204; Chung, K. W. 등, 2006. Early onset severe and late-onset mild Charcot-Marie-Tooth disease with mitofusin 2 (MFN2) mutations. Brain 129, 2103-2118; Verhoeven, K. 등, 2006. MFN2 mutation distribution and genotype/phenotype correlation in Charcot-Marie-Tooth type 2. Brain 129, 2093-2102; Feely, S. M. E. 등, 2011, MFN2 mutations cause severe phenotypes in most patients with CMT2A. Neurology 76, 1690-1696). 더 드물게, 열성 MFN2 돌연변이는 중증의 조기 발병 축삭 신경병증을 유발할 수 있다. Mfn2 돌연변이는 후근신경절 (DRG)에서 하위 운동 뉴런 및 1차 감각 뉴런에 선택적으로 독성이 있다.
MFN2의 일부 우성 돌연변이는 척수병증 또는 시신경위축을 일으키며; 이러한 복잡한 형태의 CMT2는 때때로 각각 HMSN-V 및 HMSN-VI로 지칭되지만, MFN2 돌연변이에 의해서만 유발되는 것은 아니다(Scherer, S. S. 등, 2015. Peripheral neuropathies in Rosenberg's Molecular and Genetic Basis of Neurological and Psychiatric Disease, 5th ed. Elsevier, Philadelphia, pp. 1051-1074).
포유류는 2개의 미토푸신 유전자 Mfn1 및 Mfn2를 가지고 있으며, 이는 뚜렷하지만 중첩되는 분포를 가지며, 둘 다 트랜스-상호작용을 통해 미토콘드리아 융합을 촉진할 수 있다(Chen, H., Chan, D. C., 2005. Emerging functions of mammalian mitochondrial fusion and fission. Hum. Mol. Genet. 14, R283-R289). MFN2 유전자의 거의 모든 돌연변이는 GTPase 도메인을 포함하지만, 이에 국한되지 않는 단일 점 돌연변이로 아미노산 치환을 유발한다(Cartoni, R., Martinou, J. C., 2009. Role of mitofusin 2 mutations in the physiopathology of Charcot-Marie-Tooth disease type 2A. Exp. Neurol. 218, 268-273). MFN2의 기능 상실 돌연변이는 또한 중증의 축삭 신경병증을 유발하고(Nicholson, G. A. 등, 2008. Severe early-onset axonal neuropathy with homozygous and compound heterozygous MFN2 mutations. Neurology 70, 1678-1681), 감소된 미토콘드리아 융합을 초래하기 때문에(Chen, H., Chan, D. C., 2005. Emerging functions of mammalian mitochondrial fusion and fission. Hum. Mol. Genet. 14, R283-R289), 우세한 MFN2 돌연변이는 미토콘드리아 융합에 대해 우성-음성 효과를 갖는 것이 가능하다(Detmer, S. A., Chan, D. C., 2007. Complementation between mouse Mfn1 and Mfn2 protects mitochondrial fusion defects caused by CMT2A disease mutations. J. Cell Biol. 176, 405-414: Baloh, R. H. 등, 2007. Altered axonal mitochondrial transport in the pathogenesis of Charcot-Marie-Tooth disease from mitofusin 2 mutations. J Neurosci 27, 422-430; Misko, A. 등, 2010. Mitofusin 2 is necessary for transport of axonal mitochondria and interacts with the Miro/Milton complex. J Neurosci 30, 4232-4240: Misko, A. L. 등, 2012. Mitofusin2 mutations disrupt axonal mitochondrial positioning and promote axon degeneration. J Neurosci 32, 4145-4155).
필요한 것은 CMT2A 및 관련 장애의 증상, 중증도 및/또는 진행을 감소시키는 데 유용한 치료법이다.
본 발명의 요약
인간 미토푸신 2 발현의 결함과 관련된 증상을 갖는 환자 및/또는 CMT2A를 갖는 환자를 치료하는데 유용한 바이러스 및 비-바이러스 벡터 및 조성물이 본원에 제공된다.
특정 구현예에서, AAV 캡시드 및 벡터 게놈을 포함하는 재조합 아데노-연관 바이러스(rAAV)가 제공된다. rAAV는 하기를 포함한다: (a) 인간 미토푸신 2를 암호화하는 조작된 핵산 서열; (b) (a)와 (c) 사이에 위치한 스페이서 서열; (c) (a) 및 (b)의 서열에 대해 3'에 위치한 CMT2 환자의 내인성 인간 미토푸신 2에 특이적인 적어도 하나의 miRNA 서열을 암호화하는 핵산 서열로서; 상기 (a)의 조작된 핵산 서열은 암호화된 적어도 하나의 miRNA에 대한 표적 부위가 결여되어, 암호화된 miRNA가 조작된 인간 미토푸신 2 암호화 서열을 표적화하는 것을 방지하는, 서열; 및 (c) (a) 및 (c)에 작동가능하게 연결된 조절 서열. 특정 구현예에서, 상기 AAV 캡시드는 AAV9, AAVhu68, AAV1 또는 AAVrh91로부터 선택된다. 특정 구현예에서, 상기 스페이서는 길이가 75개의 뉴클레오타이드 내지 약 250개의 뉴클레오타이드이다. 일 측면에서, 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결된 조작된 인간 미토푸신 2 암호화 서열을 포함하는 벡터가 제공된다. 특정 구현예에서, 적어도 하나의 헤어핀 miRNA를 암호화하는 핵산 서열을 포함하는 벡터가 제공되며, 상기 암호화된 miRNA는 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결된 인간 대상체의 내인성 인간 미토푸신 2에 대해 특이적이다. 특정 구현예에서, 벡터 또는 다른 조성물은 조작된 인간 미토푸신 2 암호화 서열 및 적어도 하나의 miRNA 암호화 서열 둘 다를 포함한다. 해당 구현예에서, 상기 조작된 미토푸신 2 암호화 서열은 적어도 하나의 miRNA에 대한 표적 부위가 결여되어, miRNA가 조작된 인간 미토푸신 2 암호화 서열을 표적화하는 것을 방지한다.
특정 구현예에서, 상기 벡터는 복제-결함성 바이러스 벡터이며, 이는 인간 미토푸신 2 암호화 서열, 적어도 하나의 miRNA에 대한 암호화 서열 및 조절 서열을 포함하는 벡터 게놈을 포함한다. 특정 구현예에서, 상기 바이러스 벡터는 벡터 게놈이 내부에 패키징된 AAV 캡시드를 갖는 재조합 아데노-연관 바이러스(rAAV) 입자이다. 특정 구현예에서, 상기 AAV 캡시드는 AAVhu68, AAV1 또는 AAVrh91이다.
특정 구현예에서, 서열번호 11의 핵산 서열 또는 이와 적어도 90% 동일한 서열을 갖는 조작된 미토푸신 2 암호화 서열을 포함하는 벡터가 제공되며, 단, 암호화된 miRNA에 의해 표적화되는 핵산 서열은 내인성 인간 미토푸신 2 서열과 상이하다.
특정 구현예에서, 적어도 하나의 miRNA 암호화 서열을 포함하는 핵산 서열을 포함하는 벡터가 제공되며, 이는 (a) 서열번호 15 (miR1693, 64 nt)를 포함하는 miRNA 암호화 서열; (b) 서열번호 15의 적어도 60개의 연속적인 뉴클레오타이드를 포함하는 miRNA 암호화 서열; (c) 서열번호 15와 적어도 99% 동일성을 포함하는 miRNA 암호화 서열로서, 이는 서열번호 15 (또는 서열번호 68)의 약 6개의 뉴클레오타이드 내지 약 26개의 뉴클레오타이드와 100% 동일성을 갖는 서열을 포함하는, miRNA 암호화 서열; (d) 하기 중 하나 이상을 포함하는 miRNA 암호화 서열:
(i) TTGACGTCCAGAACCTGTTCT, 서열번호 27; (ii)
AGAAGTGGGCACTTAGAGTTG, 서열번호 28; (iii)
TTCAGAAGTGGGCACTTAGAG, 서열번호 29; (iv) TTGTCAATCCAGCTGTCCAGC,
서열번호 30; (v) CAAACTTGGTCTTCACTGCAG, 서열번호 31; (vi)
AAACCTTGAGGACTACTGGAG, 서열번호 32; (vii)
TAACCATGGAAACCATGAACT, 서열번호 33; (viii)
ACAACAAGAATGCCCATGGAG, 서열번호 34; (ix)
AAAGGTCCCAGACAGTTCCTG, 서열번호 35; (x) TGTTCATGGCGGCAATTTCCT,
서열번호 36; (xi) TGAGGTTGGCTATTGATTGAC, 서열번호 37; (xii)
TTCTCACACAGTCAACACCTT, 서열번호 38; (xiii) TTTCCTCGCAGTAAACCTGCT,
서열번호 39; (xiv) AGAAATGGAACTCAATGTCTT, 서열번호 40; (xv)
TGAACAGGACATCACCTGTGA, 서열번호 41; (xvi)
AATACAAGCAGGTATGTGAAC, 서열번호 42; (xvii)
TAAACCTGCTGCTCCCGAGCC, 서열번호 43; (xviii)
TAGAGGAGGCCATAGAGCCCA, 서열번호 44; (xix)
TCTACCCGCAGGAAGCAATTG, 서열번호 45; 또는 (xx)
CTCCTTAGCAGACACAAAGAA, 서열번호 46, 또는 (i) 내지 (xx) 중 임의의 조합 중 하나 이상을 포함한다. 특정 구현예에서, 단일 핵산 분자는 인간 미토푸신 2 암호화 서열 및 miRNA 암호화 서열 둘 다를 포함하고, 상기 핵산 분자는 hMfn2 암호화 서열과 적어도 하나의 miRNA의 암호화 서열 사이에 적어도 75개의 뉴클레오타이드의 스페이서를 추가로 포함한다. 특정 구현예에서, 상기 벡터는 비-바이러스 벡터이다.
특정 구현예에서, 조성물은 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결된 조작된 인간 미토푸신 2 암호화 서열을 암호화하는 재조합 핵산 서열 및 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결된 CMT2A 환자의 내인성 인간 미토푸신 2에 특이적인 적어도 하나의 miRNA를 암호화하는 핵산 서열을 포함하며, 상기 조작된 미토푸신 2 암호화 서열은 암호화된 적어도 하나의 miRNA에 대한 표적 부위가 결여되어, miRNA가 조작된 인간 미토푸신 2 암호화 서열을 표적화하는 것을 방지한다.
특정 구현예에서, 약제학적 조성물은 벡터, rAAV, 또는 조성물, 및 약제학적으로 허용가능한 수성 현탁액, 부형제, 및/또는 희석제를 포함한다.
특정 구현예에서, 유효량의 벡터, 재조합 AAV, 또는 조성물을 이를 필요로 하는 환자에게 전달하는 것을 포함하는, 샤르코-마리-투스(CMT) 신경병증을 갖는 환자를 치료하는 방법이 제공된다. 특정 구현예에서, 유효량의 벡터, 재조합 AAV, 또는 조성물을 이를 필요로 하는 환자에게 전달하는 것을 포함하는, 샤르코-마리-투스(CMT) 신경병증을 갖는 환자에서 신경병증을 감소시키는 방법이 제공된다. 특정 구현예에서, 환자를 치료하는 방법이 제공되며, 상기 방법은 하기로부터 선택되는 하나 이상의 공동-요법과의 조합을 추가로 포함한다: 아세트아미노펜, 비스테로이드성 항염증 약물(NSAID), 삼환계 항우울제 또는 항간질 약물, 예컨대 카르바마제핀 또는 가바펜틴.
특정 구현예에서, CMT2A를 갖는 환자를 치료하기 위한 병용 요법이 제공되며, 이는 하기를 공동-투여하는 것을 포함한다: (a) 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결된 조작된 인간 미토푸신 2 암호화 서열을 암호화하는 재조합 핵산 서열로서, 상기 인간 미토푸신 2 암호화 서열은 서열번호 11의 서열 또는 이와 적어도 95% 동일한 서열을 갖고, (b)의 miRNA 표적 서열에 미스매치를 가짐에 의해 CMT2A 환자의 내인성 인간 미토푸신 2와 상이한, 재조합 핵산 서열, (b) 인간 CMT2A 대상체의 내인성 인간 미토푸신 2 서열에 특이적인 적어도 하나의 miRNA로서, 상기 mRNA는 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되는 것인, miRNA.
특정 구현예에서, CMT2A를 갖는 환자를 치료하기 위한 병용 요법이 제공되며, 이는 하기를 공동-투여하는 것을 포함한다: (a) 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결된 조작된 인간 미토푸신 2 암호화 서열을 암호화하는 재조합 핵산 서열로서, 상기 인간 미토푸신 2 암호화 서열은 (b)의 miRNA 표적 서열에 미스매치를 가짐에 의해 CMT2A 환자의 내인성 인간 미토푸신 2와 상이하도록 조작된 것인, 재조합 핵산 서열, (b) 인간 CMT2A 대상체의 내인성 인간 미토푸신 2 서열에 특이적인 적어도 하나의 miRNA로서, 상기 miRNA는 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되는 것인, miRNA. 특정 구현예에서, 제1 벡터는 핵산 (a)을 포함하고, 제2의 상이한 벡터는 적어도 하나의 miRNA (b)를 포함한다. 특정 구현예에서, 제1 벡터 및/또는 제2 벡터는 각각 동일하거나 상이할 수 있는 바이러스 벡터이다. 특정 구현예에서, 제1 및/또는 제2 벡터는 비-바이러스 벡터이다.
이들 및 다른 이점은 하기 본 발명의 상세한 설명으로부터 명백할 것이다.
도 1a 내지 1b는 미토푸신 2(Mfn2) miRNA 선택 (다양한 miRNA로 내인성 Mfn2의 넉다운)을 예시한다. 도 1a는 miRNA의 AAV-매개 전달의 정맥내 전달 후 B6 마우스의 마우스 뇌에서 qPCR에 의해 측정된, 내인성 Mfn2 RNA의 넉다운을 예시한다. 도 1b는 miRNA의 AAV-매개 전달의 정맥내 전달 후 B6 마우스의 마우스 척수에서 qPCR에 의해 측정된, 내인성 mfn2 RNA의 넉다운을 예시한다.
도 2a 내지 도 2c는 Mfn2 cDNA 전이유전자 (즉, Mfn2를 암호화하는 조작된 핵산 서열) 및 miR1518을 포함하는 AAV 벡터 전달 후 Mfn2 RNA 배수(fold) 발현을 예시하며, 상기 AAV 벡터는 마우스에 3x1011 GC의 용량으로 정맥내로 투여되었다. 도 2a는 척수에서 마우스 Mfn(mMfn2) RNA 배수 발현을 예시한다. 도 2b는 척수에서 랫트 Mfn 조작된 (rMfn2co) RNA 배수 발현을 예시한다. 도 2c는 척수에서 miR1518 RNA 배수 발현을 예시한다.
도 3은 B104 랫트 세포 중에 miRNA 처리 후 미토푸린-2 단백질의 발현 퍼센트를 측정하는 웨스턴 블롯 신호의 표시된 정량을 예시한다. 미토푸린-2 발현은 베타-액틴의 총 오버로딩(over loading) 대조군의 계산된 퍼센트 값으로부터 표시된다.
도 4는 miR1518을 포함하여 조작된 rMfn2 cDNA 전이유전자의 AAV 벡터 전달 후 처리된 마우스의 척수에서 랫트 Mfn2 (rMfn2) cDNA 발현의 배수-발현의 표시된 정량을 예시한다.
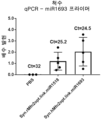
도 5는 miR1693을 포함하여 조작된 hMfn2 cDNA 전이유전자의 AAV 벡터 전달 후 처리된 마우스의 척수에서 인간 Mfn2(hMfn2) cDNA 발현의 배수-발현의 표시된 정량을 예시한다.
도 6a 및 도 6b는 마우스에서 정맥내 전달 후 AAV 벡터로부터 처리된 성숙한 miRNA의 총량을 예시한다. 도 6a는 miR1518 프라이머를 사용한 qPCR에 의해 측정된 miR1518 및 miR1693의 배수 발현을 예시한다. 도 6b는 miR1693 프라이머를 사용한 qPCR에 의해 측정된 miR1518 및 miR1693의 배수 발현을 예시한다.
도 7은 CB7 프로모터를 포함하는 다양한 벡터로 형질주입 후 Mfn2-널(null) MEF 세포주에서 Mfn2 (벡터로부터 발현된 Mfn2)의 발현 수준; CB7.CI.hMfn2.GA.WPRE.RBG; CB7.CI.hMfn2.GA.LINK.miR1518.RBG; CB7.CI.hMfn2.GA.LINK.miR538.RBG로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량으로 나타낸 발현 수준;을 나타낸다.
도 8은 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후 Mfn2-널 MEF 세포주에서 Mfn2 (벡터로부터 발현된 Mfn2)의 발현 수준; CAG.CI.hMfn2.GA.WPRE.SV40; CAG.CI.hMfn2.GA.LINK.miR1518.WPRE.SV40; CAG.CI.hMfn2.GA.LINK.miR538.WPRE.SV40. FIG로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량으로 나타낸 발현 수준;을 나타낸다.
도 9a 및 도 9b는 CB7 또는 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후 HEK293 세포주에서 Mfn2의 발현 수준을 나타낸다. 도 9a는 CB7 프로모터, (CB7.CI.hMfn2.GA.WPRE.RBG; CB7.CI.hMfn2.GA.LINK.miR1518.RBG; CB7.CI.hMfn2.GA.LINK.miR538.RBG를 포함하는 다양한 벡터로 형질주입 후, qPCR에 의해 측정되고 배수 발현으로 표시된 HEK293 세포에서의 내인성 Mfn2 넉다운을 나타낸다. 도 9b는 CAG 프로모터 CAG.CI.hMfn2.GA.WPRE.SV40; CAG.CI.hMfn2.GA.LINK.miR1518.WPRE.SV40; CAG.CI.hMfn2.GA.LINK.miR538.WPRE.SV40을 포함하는 다양한 벡터로 형질주입 후, qPCR에 의해 측정되고 배수 발현으로 표시된 HEK293 세포에서의 내인성 Mfn2 넉다운을 나타낸다.
도 10은 CB7 프로모터를 포함하는 다양한 벡터로 형질주입 후 HEK293 세포주에서 Mfn2 (내인성 Mfn2 및 벡터로부터 발현된 Mfn2)의 발현 수준; CB7.CI.hMfn2.GA.WPRE.RBG; CB7.CI.hMfn2.GA.LINK.miR1518.RBG; CB7.CI.hMfn2.GA.LINK.miR538.RBG로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량으로 나타낸 발현 수준;을 나타낸다. 정량은 발현 퍼센트로 표시되며; 형질주입 효율은 약 95%인 것으로 확인되었다.
도 11은 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후 HEK293 세포주에서 Mfn2 (내인성 Mfn2 및 벡터로부터 발현된 Mfn2)의 발현 수준; CAG.CI.hMfn2.GA.WPRE.SV40 (p6168); CAG.CI.hMfn2.GA.LINK.miR1518.WPRE.SV40 (p6169); CAG.CI.hMfn2.GA.LINK.miR538.WPRE.SV40 (p6170)으로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량으로 나타낸 발현 수준;을 나타낸다. 정량은 발현 퍼센트로 표시되며; 형질주입 효율은 약 95%인 것으로 확인되었다.
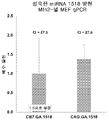
도 12a 내지 도 12c는 CB7 또는 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후, Mfn2-널 MEF 세포주 (ATCC; CRL-2933)에서 성숙한 miRNA(miR1518 또는 miR538)의 qPCR에 의해 측정된 발현 수준을 나타낸다. 도 12a는 CB7 또는 CAG 프로모터를 포함하는 벡터로 형질주입 후, Mfn2-널 MEF 세포주에서 성숙한 miR1518의 qPCR에 의해 측정되고 배수 발현으로 표시된 발현 수준의 비교를 나타낸다. 도 12b는 CB7 또는 CAG 프로모터를 포함하는 벡터로 형질주입 후, Mfn2-널 MEF 세포주에서 성숙한 miR538의 qPCR에 의해 측정되고 배수 발현으로 표시된 발현 수준의 비교를 나타낸다. 도 12c는 CB7 또는 CAG 프로모터를 포함하는 벡터로 형질주입 후, Mfn2-널 MEF 세포주에서 성숙한 miR1518 및 miR538의 qPCR에 의해 측정되고 배수 발현으로 표시된 발현 수준의 비교를 나타낸다.
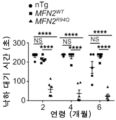
도 13a 내지 도 13f는 마우스 모델의 특성화를 나타낸다. 도 13a는 마우스 유전자형의 도식적 표현을 나타낸다. 도 13b는 웨스턴 블롯팅에 의해 측정된 뇌에서 내인성 및 FLAG-태깅된 MFN2의 상대적인 발현 수준을 특징으로 하는 마우스 표현형 특성화를 나타낸다. 도 13c는 웨스턴 블롯팅에 의해 측정된 척수에서 내인성 및 FLAG-태깅된 MFN2의 상대적인 발현 수준을 특징으로 하는 마우스 표현형 특성화를 나타낸다. 도 13d는 CMT2A 마우스 모델(nTg, MFN2WT, 및 MFN2R49Q)에서 마우스의 측정된 중량(g)을 나타낸다. 도 13e는 낙하에 대한 대기 시간(초)으로 측정된 마우스 표현형 특성화를 나타낸다. 도 13f는 악력(g)에 의해 측정된 마우스 표현형 특성화를 나타낸다.
도 14a 및 도 14b는 MFN2R94Q 마우스(연구 그룹: G1 - 야생형(WT) 마우스, PBS; G2 - MFN2R94Q 마우스, PBS; G3 - MFN2R94Q 마우스, CB7.MFN2; G4 - MFN2R94Q 마우스, CB7.MFN2.miR1518; G5 - MFN2R94Q 마우스, CB7.MFN2.miR538; G6 - MFN2R94Q 마우스, CAG.MFN2.miR1518; G7 - MFN2R94Q 마우스, CAG.MFN2.miR538)에서 약리학적 연구 결과를 나타낸다. 도 14a는 마우스 그룹 G1 내지 G7에서 측정된 체중 결과((g)으로 표시됨)를 나타낸다. 도 14b는 마우스 그룹 G1 내지 G7에서 측정된 생존 결과(0일 내지 50일에 걸친 생존 확률로 표시됨)를 나타낸다.
도 15는 MFN2R94Q 마우스에서 약리학적 연구의 악력 결과((kg)으로 표시됨)를 나타낸다.
도 2a 내지 도 2c는 Mfn2 cDNA 전이유전자 (즉, Mfn2를 암호화하는 조작된 핵산 서열) 및 miR1518을 포함하는 AAV 벡터 전달 후 Mfn2 RNA 배수(fold) 발현을 예시하며, 상기 AAV 벡터는 마우스에 3x1011 GC의 용량으로 정맥내로 투여되었다. 도 2a는 척수에서 마우스 Mfn(mMfn2) RNA 배수 발현을 예시한다. 도 2b는 척수에서 랫트 Mfn 조작된 (rMfn2co) RNA 배수 발현을 예시한다. 도 2c는 척수에서 miR1518 RNA 배수 발현을 예시한다.
도 3은 B104 랫트 세포 중에 miRNA 처리 후 미토푸린-2 단백질의 발현 퍼센트를 측정하는 웨스턴 블롯 신호의 표시된 정량을 예시한다. 미토푸린-2 발현은 베타-액틴의 총 오버로딩(over loading) 대조군의 계산된 퍼센트 값으로부터 표시된다.
도 4는 miR1518을 포함하여 조작된 rMfn2 cDNA 전이유전자의 AAV 벡터 전달 후 처리된 마우스의 척수에서 랫트 Mfn2 (rMfn2) cDNA 발현의 배수-발현의 표시된 정량을 예시한다.
도 5는 miR1693을 포함하여 조작된 hMfn2 cDNA 전이유전자의 AAV 벡터 전달 후 처리된 마우스의 척수에서 인간 Mfn2(hMfn2) cDNA 발현의 배수-발현의 표시된 정량을 예시한다.
도 6a 및 도 6b는 마우스에서 정맥내 전달 후 AAV 벡터로부터 처리된 성숙한 miRNA의 총량을 예시한다. 도 6a는 miR1518 프라이머를 사용한 qPCR에 의해 측정된 miR1518 및 miR1693의 배수 발현을 예시한다. 도 6b는 miR1693 프라이머를 사용한 qPCR에 의해 측정된 miR1518 및 miR1693의 배수 발현을 예시한다.
도 7은 CB7 프로모터를 포함하는 다양한 벡터로 형질주입 후 Mfn2-널(null) MEF 세포주에서 Mfn2 (벡터로부터 발현된 Mfn2)의 발현 수준; CB7.CI.hMfn2.GA.WPRE.RBG; CB7.CI.hMfn2.GA.LINK.miR1518.RBG; CB7.CI.hMfn2.GA.LINK.miR538.RBG로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량으로 나타낸 발현 수준;을 나타낸다.
도 8은 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후 Mfn2-널 MEF 세포주에서 Mfn2 (벡터로부터 발현된 Mfn2)의 발현 수준; CAG.CI.hMfn2.GA.WPRE.SV40; CAG.CI.hMfn2.GA.LINK.miR1518.WPRE.SV40; CAG.CI.hMfn2.GA.LINK.miR538.WPRE.SV40. FIG로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량으로 나타낸 발현 수준;을 나타낸다.
도 9a 및 도 9b는 CB7 또는 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후 HEK293 세포주에서 Mfn2의 발현 수준을 나타낸다. 도 9a는 CB7 프로모터, (CB7.CI.hMfn2.GA.WPRE.RBG; CB7.CI.hMfn2.GA.LINK.miR1518.RBG; CB7.CI.hMfn2.GA.LINK.miR538.RBG를 포함하는 다양한 벡터로 형질주입 후, qPCR에 의해 측정되고 배수 발현으로 표시된 HEK293 세포에서의 내인성 Mfn2 넉다운을 나타낸다. 도 9b는 CAG 프로모터 CAG.CI.hMfn2.GA.WPRE.SV40; CAG.CI.hMfn2.GA.LINK.miR1518.WPRE.SV40; CAG.CI.hMfn2.GA.LINK.miR538.WPRE.SV40을 포함하는 다양한 벡터로 형질주입 후, qPCR에 의해 측정되고 배수 발현으로 표시된 HEK293 세포에서의 내인성 Mfn2 넉다운을 나타낸다.
도 10은 CB7 프로모터를 포함하는 다양한 벡터로 형질주입 후 HEK293 세포주에서 Mfn2 (내인성 Mfn2 및 벡터로부터 발현된 Mfn2)의 발현 수준; CB7.CI.hMfn2.GA.WPRE.RBG; CB7.CI.hMfn2.GA.LINK.miR1518.RBG; CB7.CI.hMfn2.GA.LINK.miR538.RBG로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량으로 나타낸 발현 수준;을 나타낸다. 정량은 발현 퍼센트로 표시되며; 형질주입 효율은 약 95%인 것으로 확인되었다.
도 11은 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후 HEK293 세포주에서 Mfn2 (내인성 Mfn2 및 벡터로부터 발현된 Mfn2)의 발현 수준; CAG.CI.hMfn2.GA.WPRE.SV40 (p6168); CAG.CI.hMfn2.GA.LINK.miR1518.WPRE.SV40 (p6169); CAG.CI.hMfn2.GA.LINK.miR538.WPRE.SV40 (p6170)으로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량으로 나타낸 발현 수준;을 나타낸다. 정량은 발현 퍼센트로 표시되며; 형질주입 효율은 약 95%인 것으로 확인되었다.
도 12a 내지 도 12c는 CB7 또는 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후, Mfn2-널 MEF 세포주 (ATCC; CRL-2933)에서 성숙한 miRNA(miR1518 또는 miR538)의 qPCR에 의해 측정된 발현 수준을 나타낸다. 도 12a는 CB7 또는 CAG 프로모터를 포함하는 벡터로 형질주입 후, Mfn2-널 MEF 세포주에서 성숙한 miR1518의 qPCR에 의해 측정되고 배수 발현으로 표시된 발현 수준의 비교를 나타낸다. 도 12b는 CB7 또는 CAG 프로모터를 포함하는 벡터로 형질주입 후, Mfn2-널 MEF 세포주에서 성숙한 miR538의 qPCR에 의해 측정되고 배수 발현으로 표시된 발현 수준의 비교를 나타낸다. 도 12c는 CB7 또는 CAG 프로모터를 포함하는 벡터로 형질주입 후, Mfn2-널 MEF 세포주에서 성숙한 miR1518 및 miR538의 qPCR에 의해 측정되고 배수 발현으로 표시된 발현 수준의 비교를 나타낸다.
도 13a 내지 도 13f는 마우스 모델의 특성화를 나타낸다. 도 13a는 마우스 유전자형의 도식적 표현을 나타낸다. 도 13b는 웨스턴 블롯팅에 의해 측정된 뇌에서 내인성 및 FLAG-태깅된 MFN2의 상대적인 발현 수준을 특징으로 하는 마우스 표현형 특성화를 나타낸다. 도 13c는 웨스턴 블롯팅에 의해 측정된 척수에서 내인성 및 FLAG-태깅된 MFN2의 상대적인 발현 수준을 특징으로 하는 마우스 표현형 특성화를 나타낸다. 도 13d는 CMT2A 마우스 모델(nTg, MFN2WT, 및 MFN2R49Q)에서 마우스의 측정된 중량(g)을 나타낸다. 도 13e는 낙하에 대한 대기 시간(초)으로 측정된 마우스 표현형 특성화를 나타낸다. 도 13f는 악력(g)에 의해 측정된 마우스 표현형 특성화를 나타낸다.
도 14a 및 도 14b는 MFN2R94Q 마우스(연구 그룹: G1 - 야생형(WT) 마우스, PBS; G2 - MFN2R94Q 마우스, PBS; G3 - MFN2R94Q 마우스, CB7.MFN2; G4 - MFN2R94Q 마우스, CB7.MFN2.miR1518; G5 - MFN2R94Q 마우스, CB7.MFN2.miR538; G6 - MFN2R94Q 마우스, CAG.MFN2.miR1518; G7 - MFN2R94Q 마우스, CAG.MFN2.miR538)에서 약리학적 연구 결과를 나타낸다. 도 14a는 마우스 그룹 G1 내지 G7에서 측정된 체중 결과((g)으로 표시됨)를 나타낸다. 도 14b는 마우스 그룹 G1 내지 G7에서 측정된 생존 결과(0일 내지 50일에 걸친 생존 확률로 표시됨)를 나타낸다.
도 15는 MFN2R94Q 마우스에서 약리학적 연구의 악력 결과((kg)으로 표시됨)를 나타낸다.
인간 미토푸신 2 (또는 hMfn2) 단백질을 발현하는 핵산 서열 및 표적 부위가 조작된 인간 미토푸신 2 암호화 서열에 존재하지 않는 환자의 내인성 인간 미토푸신 2 유전자 내의 부위를 특이적으로 표적화하는 적어도 하나의 miRNA를 암호화하는 핵산 서열을 환자에게 공동-투여하기 위한 서열, 벡터 및 조성물이 본원에 제공된다. 적합하게는, 인간 미토푸신 2 암호화 서열은 암호화된 miRNA에 대한 특이적인 표적 부위를 제거하도록 조작된다. 신규 조작된 인간 미토푸신 2 암호화 서열 및 신규 miRNA 서열이 본원에 제공된다. 이들은 CMT2A의 치료를 위해 단독으로 또는 서로 및/또는 다른 치료제와 조합하여 사용될 수 있다.
본원에서 사용된 바와 같이, 용어 "내인성 미토푸신 2"는 CMT2A를 갖는 인간에서 미토푸신 2 단백질을 암호화하는 미토푸신 2 유전자를 지칭한다. CMT2A를 갖는 환자는 다수의 미스센스 돌연변이 또는 대립형질 변이를 가질 수 있다. 또한, 다양한 대립형질 변이를 기술하는, omim.org/allelicVariants/608507을 참조한다. 상염색체 우성 샤르코-마리-투스(CMT) 질환 유형 2A2A(CMT2A2A)는 염색체 1p36.2 상의 MFN2 유전자(608507)에서의 이형접합 돌연변이에 의해 유발된다. MFN2 유전자의 동형접합 또는 복합 이형접합 돌연변이는 더 초기에 발병하는 더 중증 장애인, 상염색체 열성 CMT2A2B(617087)를 유발한다. 염색체 1p36.2에 매핑되는 또 다른 형태의 CMT2A인 CMT2A1(118210)은 KIF1B 유전자(605995)의 돌연변이에 의해 유발된다. 또한, 중첩되는 특징을 가진 대립형질 장애인, 유전성 운동 및 감각 신경병증 VI(HMSN6; 601152)를 참조한다.
CMT2A가 없는 환자에서 내인성으로 발견되는 것과 같은 천연의, 기능성의, 인간 Mfn2a 유전자는 서열번호 18로 복제되고, 천연의, 기능성의, 인간 Mf2A 단백질서열번호 19로 복제된다. 미토푸신 2는 근육, 척수, 및 뇌와 척수를 근육에 그리고 촉각, 통증, 열, 및 소리와 같은 감각을 감지하는 감각세포에 연결하는 신경(말초 신경)을 포함한, 많은 유형의 세포 및 조직에서 만들어진다. 이 유전자는 대안적으로 칭해질 수 있다: CMT2A2, CRPP1, KIAA0214, MARF, MFN2_Human 또는 미토콘드리아 조립 조절 인자. 2020년 7월 12일자로 접속된 OMIM.ORG/entry/609260을 참조한다. 특정 구현예에서, 서열번호 19의 아미노산 서열과 100% 미만의 동일성을 갖는 기능성 Mfn2 단백질은 본원에 제공되는 조성물(예를 들어, 서열번호 19와 97% 내지 100% 동일성을 갖는 Mfn2)에 의해 전달될 수 있다. 해당 구현예에서, 천연 기능성 인간 Mfn2의 효소적 및 결합 기능은 바람직하게는 유지된다. 또한, UniProtKB-09140(예를 들어, 위치 305 및 307의 결합 부위가 보존되고/되거나 뉴클레오타이드 106-111 및/또는 258-261의 뉴클레오타이드 결합 부위가 보존됨)을 참조한다.
일 구현예에서, 조작된 미토푸신 2 암호화 서열이 제공되며, 이는 서열번호 11의 핵산 서열 또는 서열번호 11과 약 90%, 적어도 95% 동일, 적어도 97% 동일, 적어도 98% 동일, 또는 99% 내지 100% 동일한 서열을 갖고, 이는 비-CMT2A 환자에서 발견되는 인간 미토푸신 2 단백질을 발현한다. 예를 들어, 서열번호 19를 참조한다. 또한, 서열번호 2 및 서열번호 4를 참조한다.
특정 구현예에서, 서열번호 11의 핵산 서열 또는 적어도 80% 동일한 서열을 갖는 조작된 미토푸신 2 암호화 서열이 제공되며, 단, 서열번호 11의 nt 216 내지 236은, 예를 들어, 조작된 암호화 서열이 miR538 암호화 서열과 공동-투여되는 경우에 보존된다(예를 들어, 100% 동일 또는 적어도 99% 동일).
특정 구현예에서, 서열번호 11의 핵산 서열 또는 적어도 80% 동일한 서열을 갖는 조작된 미토푸신 2 암호화 서열이 제공되며, 단, 서열번호 11의 nt 1371 내지 1391은, 예를 들어, 조작된 암호화 서열이 miR1518 암호화 서열과 공동-투여되는 경우에 보존된다(예를 들어, 100% 동일 또는 적어도 99% 동일). 적합하게는, 서열번호 11과 동일성을 갖는 서열은 동일한 단백질을 발현한다. 예를 들어, 서열번호 19; 서열번호 2 및 서열번호 4를 참조한다.
일 구현예에서, 서열번호 28의 핵산 서열 또는 서열번호 24와 적어도 90%, 적어도 95% 동일, 적어도 97% 동일, 적어도 98% 동일, 적어도 99% 동일, 및/또는 적어도 99% 내지 100% 동일한 서열을 갖는 조작된 미토푸신 2 암호화 서열이 제공된다.
"5' UTR"은 유전자 산물 암호화 서열에 대한 개시 코돈의 업스트림이다. 5' UTR은 일반적으로 3' UTR보다 더 짧다. 일반적으로, 5' UTR은 길이가 약 3개의 뉴클레오타이드 내지 약 200개의 뉴클레오타이드이지만, 선택적으로 더 길 수 있다.
"3' UTR"은 유전자 산물에 대한 암호화 서열의 다운스트림이며, 일반적으로 5' UTR보다 더 길다. 특정 구현예에서, 3' UTR은 길이가 약 200개의 뉴클레오타이드 내지 약 800개의 뉴클레오타이드이지만, 선택적으로 더 길거나 더 짧을 수 있다.
본원에서 사용된 바와 같이, "miRNA"는 mRNA를 조절하고 단백질로 번역되는 것을 중지시키는 작은 비-암호화 RNA 분자인 마이크로RNA를 지칭한다. 일반적으로, 헤어핀-형성 RNA는 루프(loop) 서열에 의해 안티센스 가닥(예를 들어, 가이드 가닥)에 연결된 센스 가닥(예를 들어, 패신저 가닥)을 포함하는 듀플렉스를 가지는 스템 부분을 암호화하는 단일 핵산을 함유하는 자가-상보적 "스템-루프" 구조를 갖는다. 패신저 가닥 및 가이드 가닥은 상보성을 공유한다. 일부 구현예에서, 패신저 가닥 및 가이드 가닥은 100% 상보성을 공유한다. 일부 구현예에서, 패신저 가닥 및 가이드 가닥은 적어도 50%, 적어도 60%, 적어도 70%, 적어도 80%, 적어도 90%, 적어도 95%, 또는 적어도 99% 상보성을 공유한다. 패신저 가닥 및 가이드 가닥은 염기쌍 미스매치로 인해 상보성이 결여될 수 있다. 일부 구현예에서, 헤어핀-형성 RNA의 패신저 가닥 및 가이드 가닥은 적어도 1개, 적어도 2개, 적어도 3개, 적어도 4개, 적어도 5개, 적어도 6개, 적어도 7개, 적어도 8개, 적어도 9개, 또는 적어도 10개의 미스매치를 갖는다. 일반적으로, (루프 대비) 스템의 처음 2-8개의 뉴클레오타이드는 "시드(seed)" 잔기로 지칭되고, 표적 인식 및 결합에서 중요한 역할을 한다. (루프 대비) 스템의 첫 번째 잔기는 "앵커" 잔기로 지칭된다. 일부 구현예에서, 헤어핀-형성 RNA는 앵커 잔기에서 미스매치를 갖는다. 본원에서 사용된 바와 같이, miRNA는 (예를 들어, 내인성 hMfn2에서) 상보적 염기쌍 형성에 의해 mRNA에 특이적으로 결합하여, mRNA의 파괴 또는 침묵을 유발하는 뉴클레오타이드의 영역인 "시드 서열"을 포함한다. 이러한 침묵은 내인성 hMfn2의 완전한 소실보다는 하향 조절을 초래할 수 있다. 달리 명시되지 않는 한, 용어 "miRNA"는 인공적으로 설계된 인공 마이크로RNA(amiRNA)를 포괄한다.
"자가-상보적 핵산"은 핵산 가닥 내의 뉴클레오타이드의 상보성(예를 들어, 염기쌍 형성)으로 인해, 자체적으로 혼성화(즉, 자체적으로 폴딩)되어 단일-가닥 듀플렉스 구조를 형성할 수 있는 핵산을 지칭한다. 자가-상보적 핵산은 다양한 2차 구조, 예컨대 헤어핀 루프, 루프, 돌출부, 접합부 및 내부 돌출부를 형성할 수 있다. 특정 자가-상보적 핵산(예를 들어, miRNA 또는 AmiRNA)은 조절 기능, 예컨대 유전자 침묵을 수행한다.
본원에서 제공되는 암호화된 miRNA는 CMT2A를 갖는 환자의 내인성 인간 미토푸신 2 유전자를 특이적으로 표적화하도록 설계되었다. 특정 구현예에서, miRNA 암호화 서열은 하기 표 1의 안티-센스 서열, 서열번호 27-46, 68 및 89를 포함한다.
표 1.
특정 구현예에서, 시드 서열은 표에 기술된 안티센스 서열과 100% 동일하다. 특정 구현예에서, 시드 서열은 성숙한 miRNA(5'에서 3'으로)에 위치하고, 길이가 더 길 수 있지만, 일반적으로 miRNA 중 miRNA 센스 가닥의 5' 말단으로부터 (센스 (+) 가닥의 5' 말단으로부터) 2 내지 7개, 2 내지 8개 또는 약 6개의 뉴클레오타이드 위치에서 시작한다. 특정 구현예에서, 시드 서열의 길이는 miRNA 서열 길이의 약 30% 이상이며, 길이가 적어도 7개의 뉴클레오타이드 내지 약 28개의 뉴클레오타이드, 길이가 적어도 8개의 뉴클레오타이드 내지 약 28개의 뉴클레오타이드, 7개의 뉴클레오타이드 내지 28개의 뉴클레오타이드, 8개의 뉴클레오타이드 내지 18개의 뉴클레오타이드, 길이가 12개의 뉴클레오타이드 내지 28개의 뉴클레오타이드, 약 20개 내지 약 26개의 뉴클레오타이드, 약 21개의 뉴클레오타이드, 약 24개의 뉴클레오타이드, 또는 약 26개의 뉴클레오타이드일 수 있다. 본원에 제공된 예에서, miRNA는 예를 들어, 길이가 약 50개 내지 약 80개의 뉴클레오타이드, 또는 약 55개의 뉴클레오타이드 내지 약 70개의 뉴클레오타이드, 또는 길이가 60개 내지 65개의 뉴클레오타이드인, 스템-루프 miRNA 전구체 서열의 형태로 전달된다. 특정 구현예에서, 이 miRNA 전구체는 약 5개의 뉴클레오타이드, 약 21개의 뉴클레오타이드 시드 서열, 약 19개의 뉴클레오타이드 스템 루프 및 약 19개의 뉴클레오타이드 센스 서열을 포함하고, 상기 센스 서열은 미스매치되는 1개 또는 2개의 뉴클레오타이드를 가진 안티-센스 서열에 상응한다. 적합한 miRNA 암호화 서열의 예는 서열번호 15의 miR1693 서열이다. 특정 구현예에서, miRNA 암호화 서열은 서열번호 15 (miR1693, 64 nt); 서열번호 15의 적어도 60개의 연속적인 뉴클레오타이드를 포함하는 miRNA 암호화 서열; 또는 서열번호 15와 적어도 99% 동일성을 포함하는 miRNA 암호화 서열로서, 이는 서열번호 15 (또는 서열번호 68)의 약 6개의 뉴클레오타이드 내지 약 26개의 뉴클레오타이드와 100% 동일성을 갖는 서열을 포함하는, miRNA 암호화 서열을 포함한다. 특정 구현예에서, 상기 표의 다른 서열은 서열번호 15 (또는 서열번호 68)의 6번 내지 26번 위치에서 치환될 수 있다. 또 다른 구현예에서, 서열번호 15의 6번 내지 26번 위치가 유지되고, 대안적인 서열은 스템-루프 서열에 대해 선택된다. 특정 구현예에서, miRNA 암호화 서열은 서열번호 16 (miR1518, 59 nt), 서열번호 16과 적어도 99% 동일성을 포함하는 서열을 포함한다. 특정 구현예에서, miRNA 암호화 서열은 서열번호 89 (miR538, 59 nt), 또는 서열번호 89와 적어도 99% 동일성을 포함하는 서열을 포함한다. 특정 구현예에서, 대안적인 스템-루프 서열이 선택되고, 상기 스템의 안티센스 가닥은 서열번호 16의 nt 6 내지 26, 또는 서열번호 89의 nt 1 내지 21이고, 상기 루프 서열은 서열번호 41의 nt 27 내지 45 또는 서열번호 89의 nt 22 내지 40이다.
특정 구현예에서, 핵산 분자(예를 들어, 발현 카세트 또는 벡터 게놈)는 하나 이상의 miRNA 암호화 서열을 함유할 수 있다. 상기는 (a) 서열번호 15 (miR1693, 64 nt)를 포함하는 miRNA 암호화 서열; (b) 서열번호 15의 적어도 60개의 연속적인 뉴클레오타이드를 포함하는 miRNA 암호화 서열; (c) 서열번호 15와 적어도 99% 동일성을 포함하는 miRNA 암호화 서열로서, 이는 서열번호 15 (또는 서열번호 68)의 약 6개의 뉴클레오타이드 내지 약 26개의 뉴클레오타이드와 100% 동일성을 갖는 서열을 포함하는, miRNA 암호화 서열; 및/또는 (d) 하기 중 하나 이상을 포함하는 miRNA 암호화 서열:
(i) TTGACGTCCAGAACCTGTTCT, 서열번호 27; (ii)
AGAAGTGGGCACTTAGAGTTG, 서열번호 28; (iii)
TTCAGAAGTGGGCACTTAGAG, 서열번호 29; (iv) TTGTCAATCCAGCTGTCCAGC,
서열번호 30; (v) CAAACTTGGTCTTCACTGCAG, 서열번호 31; (vi)
AAACCTTGAGGACTACTGGAG, 서열번호 32; (vii)
TAACCATGGAAACCATGAACT, 서열번호 33; (viii)
ACAACAAGAATGCCCATGGAG, 서열번호 34; (ix)
AAAGGTCCCAGACAGTTCCTG, 서열번호 35; (x) TGTTCATGGCGGCAATTTCCT,
서열번호 36; (xi) TGAGGTTGGCTATTGATTGAC, 서열번호 37; (xii)
TTCTCACACAGTCAACACCTT, 서열번호 38; (xiii) TTTCCTCGCAGTAAACCTGCT,
서열번호 39; (xiv) AGAAATGGAACTCAATGTCTT, 서열번호 40; (xv)
TGAACAGGACATCACCTGTGA, 서열번호 41; (xvi)
AATACAAGCAGGTATGTGAAC, 서열번호 42; (xvii)
TAAACCTGCTGCTCCCGAGCC, 서열번호 43; (xviii)
TAGAGGAGGCCATAGAGCCCA, 서열번호 44; (xix)
TCTACCCGCAGGAAGCAATTG, 서열번호 45; 또는 (xx)
CTCCTTAGCAGACACAAAGAA, 서열번호 46, 또는 (i) 내지 (xx) 중 임의의 조합 중 1개, 2개 또는 그 초과의 서열을 갖는 miRNA 암호화 서열을 포함할 수 있다. 특정 구현예에서, 핵산 분자(예를 들어, 발현 카세트 또는 벡터 게놈)는 서열번호 16 (miR1518)의 1개, 2개 또는 그 초과의 miRNA 암호화 서열을 함유할 수 있다. 특정 구현예에서, 핵산 분자(예를 들어, 발현 카세트 또는 벡터 게놈)는 서열번호 89 (miR538)의 1개, 2개 또는 그 초과의 miRNA 암호화 서열을 함유할 수 있다.
본원에서 사용된 바와 같이, "miRNA 표적 서열"은 (예를 들어, hMfn2의) DNA 양성 가닥(5'에서 3'으로)에 위치한 서열이고, 상기 miRNA 시드 서열을 포함하는 miRNA 서열에 적어도 부분적으로 상보적이다. 상기 miRNA 표적 서열은 암호화된 전이유전자 산물의 비번역 영역에 대해 외인성이며, 전이유전자 발현의 억제가 요구되는 세포에서 miRNA에 의해 특이적으로 표적화되도록 설계된다. 이론에 구속시키고자 하는 것은 아니지만, hMfn2는 유비쿼터스 단백질이며 과도한 발현이 독성 및/또는 다른 부정적인 부작용과 연관될 수 있기 때문에, 상기 miRNA는 CMT2A 환자에 전달되는 조작된 hMfn2 유전자를 표적화하는 것을 피하면서 내인성 hMfn2 유전자를 우선적으로 표적화한다. 보다 구체적으로, 벡터를 통해 전달되는 hMfn2를 암호화하는 서열은 표적 부위에 변경된 코돈 서열을 포함하도록 설계된다.
전형적으로, miRNA 표적 서열은 길이가 적어도 7개의 뉴클레오타이드 내지 약 28개의 뉴클레오타이드, 길이가 적어도 8개의 뉴클레오타이드 내지 약 28개의 뉴클레오타이드, 7개의 뉴클레오타이드 내지 28개의 뉴클레오타이드, 8개의 뉴클레오타이드 내지 18개의 뉴클레오타이드, 길이가 12개의 뉴클레오타이드 내지 28개의 뉴클레오타이드, 약 20개 내지 약 26개의 뉴클레오타이드, 약 22개의 뉴클레오타이드, 약 24개의 뉴클레오타이드, 또는 약 26개의 뉴클레오타이드이고, miRNA 시드 서열에 상보적인 적어도 하나의 연속적인 영역 (예를 들어, 7개 또는 8개의 뉴클레오타이드)을 함유한다. 특정 구현예에서, 표적 서열은 일부 미스매치가 있는 miRNA 시드 서열과 정확한 상보성(100%) 또는 부분적 상보성을 갖는 서열을 포함한다. 특정 구현예에서, 표적 서열은 miRNA 시드 서열과 100% 상보성인 적어도 7개 내지 8개의 뉴클레오타이드를 포함한다. 특정 구현예에서, 표적 서열은 miRNA 시드 서열과 100% 상보적인 서열로 이루어진다. 특정 구현예에서, 표적 서열은 시드 서열과 100% 상보적인 서열의 다중 카피(에를 들어, 2개 또는 3개의 카피)를 함유한다. 특정 구현예에서, 100% 상보성의 영역은 표적 서열 길이의 적어도 30%를 포함한다. 특정 구현예에서, 표적 서열의 나머지는 miRNA와 적어도 약 80% 내지 약 99% 상보성을 갖는다. 특정 구현예에서, DNA 양성 가닥을 함유한 발현 카세트에서, miRNA 표적 서열은 miRNA의 역상보체이다.
따라서, 서열번호 11 및 24의 Mfn2 암호화 서열과 95% 내지 99.9% 동일한 본원에서 제공되는 서열은 작제물에서 선택된 miRNA가 표적으로 하는 천연 인간 서열로 되돌아가는 것을 방지하도록 설계된다.
특정 구현예에서, 상기 miRNA는 조작된 hMfn2 유전자를 표적화하는 것을 피하면서 내인성 hMfn2 유전자를 우선적으로 표적화하며, 상기 내인성 hMfn2 핵산 서열은 서열번호 18이다. 특정 구현예에서, miRNA 암호화 서열은 (i) 서열번호 18의 nt 216-236을 표적화하는, TTGACGTCCAGAACCTGTTCT, 서열번호 27; (ii) 서열번호 18의 nt 552-572를 표적화하는, AGAAGTGGGCACTTAGAGTTG, 서열번호 28; (iii) 서열번호 18의 nt 555-575를 표적화하는, TTCAGAAGTGGGCACTTAGAG, 서열번호 29; (iv) 서열번호 18의 nt 624-644를 표적화하는, TTGTCAATCCAGCTGTCCAGC, 서열번호 30; (v) 서열번호 18의 nt 1364-1384를 표적화하는, CAAACTTGGTCTTCACTGCAG, 서열번호 31; (vi) 서열번호 18의 nt 1055-1075를 표적화하는, AAACCTTGAGGACTACTGGAG, 서열번호 32; (vii) 서열번호 18의 nt 1793-1813을 표적화하는, TAACCATGGAAACCATGAACT, 서열번호 33; (viii) 서열번호 18의 nt 1842-1862를 표적화하는, ACAACAAGAATGCCCATGGAG, 서열번호 34; (ix) 서열번호 181의 nt 2068-2088을 표적화하는, AAAGGTCCCAGACAGTTCCTG, 서열번호 35; (x) 서열번호 18의 nt 2135-2155를 표적화하는, TGTTCATGGCGGCAATTTCCT, 서열번호 36; (xi) 5'UTR을 표적화하는, TGAGGTTGGCTATTGATTGAC, 서열번호 37; (xii) 3'UTR을 표적화하는, TTCTCACACAGTCAACACCTT, 서열번호 38; (xiii) 서열번호 18의 nt 1157- 1177을 표적화하는, TTTCCTCGCAGTAAACCTGCT, 서열번호 39; (xiv) 서열번호 18의 nt 1616-1636을 표적화하는, AGAAATGGAACTCAATGTCTT, 서열번호 40; (xv) 3'UTR을 표적화하는, TGAACAGGACATCACCTGTGA, 서열번호 41; (xvi) 3'UTR을 표적화하는, AATACAAGCAGGTATGTGAAC, 서열번호 42; (xvii) 서열번호 18의 nt 1146-1166을 표적화하는, TAAACCTGCTGCTCCCGAGCC, 서열번호 43; (xviii) 서열번호 18의 nt 1914-1934를 표적화하는, TAGAGGAGGCCATAGAGCCCA, 서열번호 44; (xix) 서열번호 18의 nt 390-410을 표적화하는, TCTACCCGCAGGAAGCAATTG, 서열번호 45; 또는 (xx) 서열번호 18의 nt 904-924를 표적화하는, CTCCTTAGCAGACACAAAGAA, 서열번호 46 중 하나 이상을 포함한다.
특정 구현예에서, 상기 조작된 hMfn2 핵산 서열은 서열번호 11 또는 24이다. 특정 구현예에서, 상기 조작된 hMfn2 핵산 서열은 서열번호 18이며, 상기 1개, 2개, 3개, 또는 4개의 뉴클레오타이드 미스매치가 하기 뉴클레오타이드의 영역에 존재한다: (i) 서열번호 18의 nt 216-236; (ii) 서열번호 18의 nt 552-572; (iii) 서열번호 18의 nt 555- 575; (iv) 서열번호 18의 nt 624-644; (v) 서열번호 18의 nt 1055-1075; (vi) 서열번호 18의 nt 1364-1384; (vii) 서열번호 18의 nt 1793-1813; (viii) 서열번호 18의 nt 1842-1862; (ix) 서열번호 18의 nt 2068-2088; (x) 서열번호 18의 nt 2135-2155; (xi) 서열번호 18의 nt 1157-1177; (xii) 서열번호 18의 nt 1616-1636; (xiii) 서열번호 18의 nt 1146-1166; (xiv) 서열번호 18의 nt 1914-1934; (xv) 서열번호 18의 nt 390-410; 또는 (xvi) 서열번호 18의 nt 904-924.
특정 구현예에서, 단일 핵산 (예를 들어, 이를 포함하는 발현 카세트 또는 벡터 게놈)은 조작된 hMfn2 암호화 서열 및 적어도 하나의 miRNA 암호화 서열 둘 다를 포함하고, 상기 miRNA는 조작된 hMfn2 서열에 존재하지 않는 내인성 인간 Mfn2 서열의 영역을 특이적으로 표적화한다. 특정 구현예에서, 인간 미토푸신 2 암호화 서열은 상기 적어도 하나의 miRNA의 업스트림 (5')이고, 이들 두 요소는 스페이서 또는 링커 서열에 의해 분리된다. 특정 구현예에서, hMfn2 암호화 서열의 정지 코돈과 대부분의 5' miRNA 암호화 서열의 시작 사이에는 적어도 75개의 뉴클레오타이드가 있다. 특정 구현예에서, 상기 스페이서는 약 75개의 뉴클레오타이드 내지 약 300개의 뉴클레오타이드, 또는 약 75개의 뉴클레오타이드 내지 약 250개의 뉴클레오타이드, 또는 약 75개의 뉴클레오타이드 내지 약 200개의 뉴클레오타이드, 또는 약 75개의 뉴클레오타이드 내지 약 150개의 뉴클레오타이드, 또는 약 75개의 뉴클레오타이드 내지 약 100개의 뉴클레오타이드, 또는 약 80개의 뉴클레오타이드 내지 약 300개의 뉴클레오타이드, 또는 약 80개의 뉴클레오타이드 내지 약 250개의 뉴클레오타이드, 또는 약 80개의 뉴클레오타이드 내지 약 200개의 뉴클레오타이드, 또는 약 80개의 뉴클레오타이드 내지 약 150개의 뉴클레오타이드, 또는 약 80개의 뉴클레오타이드 내지 약 100개의 뉴클레오타이드이다. 선택적으로, 조작된 hMfn2 암호화 서열 및 적어도 하나의 miRNA 암호화 서열은 약 75개의 뉴클레오타이드에 의해 분리된다. 적합하게는, 스페이서 서열은 임의의 제한 효소 부위가 결여된 비-암호화 서열이다. 선택적으로 스페이서는 하나 이상의 인트론 서열을 포함할 수 있다. 특정 구현예에서, 하나 이상의 miRNA 서열은 인트론 내에 위치할 수 있다. 특정 구현예에서, 링커 서열은 서열번호 17이다. 특정 구현예에서, 링커 서열은 서열번호 90이다.
특정 구현예에서, 조작된 hMfn2 암호화 서열 및 miRNA 암호화 서열(들)은 상이한 핵산 서열, 예를 들어 2개 이상의 상이한 벡터, 벡터 및 LNP를 포함하는 조합 등을 통해 전달된다. 특정 구현예에서, 2개의 상이한 벡터는 AAV 벡터이다. 특정 구현예에서, 이들 벡터는 상이한 발현 카세트를 갖는다. 다른 구현예에서, 이들 벡터는 동일한 캡시드를 갖는다. 다른 구현예에서, 벡터는 상이한 구현예를 갖는다. 특정 구현예에서, miRNA 암호화 서열(들)은 LNP 또는 다른 비-바이러스 전달 시스템을 통해 전달된다. 특정 구현예에서, 조작된 hMfn2 서열은 LNP 또는 다른 비-바이러스 전달 시스템을 통해 전달된다. 특정 구현예에서, 2개 이상의 상이한 전달 시스템 (예를 들어, 바이러스 및 비-바이러스, 2개의 상이한 비-바이러스)의 조합이 사용된다. 이들 및 다른 구현예에서, 2개 이상의 상이한 벡터 또는 다른 전달 시스템은 실질적으로 동시에 투여될 수 있거나, 이들 시스템 중 하나 이상이 다른 것보다 먼저 전달될 수 있다. 특정 구현예에서, 조작된 hMfn2 서열은 서열번호 11, 또는 이와 90% 내지 100% 동일한 서열이며, 이는 hMfn2를 암호화하고 공동-투여되는 miR에 결합하지 않는 mRNA를 암호화한다. 특정 구현예에서, 조작된 hMfn2 서열은 서열번호 24, 또는 이와 90% 내지 100% 동일한 서열이며, 이는 hMfn2를 암호화하고 공동-투여되는 miR에 결합하지 않는 mRNA를 암호화한다. 특정 구현예에서, miR은 대상체에서 내인성 hMfn2를 표적으로 하지만, 조작된 hMfn2 cDNA 서열 또는 조작된 암호화된 mRNA 서열을 표적으로 하지 않는 서열번호 89의 서열을 갖는 miR538이다.
본원에서 사용된 바와 같이, 용어 "AAV.hMfn2" 또는 "rAAV.hMfn2"는 조절 서열의 제어 하에 인간 미토푸신 2 암호화 서열 (예를 들어, cDNA)을 포함하는 벡터 게놈을 내부에 가지는 AAV 캡시드를 갖는 재조합 아데노-연관 바이러스를 지칭하는데 사용된다. 본원에서 사용된 바와 같이, 용어 "AAV.hMfn2 miRXXX" 또는 "rAAV.hMfn2.miRXXX"는 내인성 인간 미토푸신 2 암호화 서열을 표적화하는 miR을 포함하는 벡터 게놈을 내부에 가지는 AAV 캡시드를 갖는 재조합 아데노-연관 바이러스를 지칭하는데 사용된다.
예를 들어, AAV1 캡시드를 갖는 재조합 AAV를 지칭하는 AAV1.hMfn2 또는 rAAV1.hMfn2; AAVhu68 캡시드를 갖는 재조합 AAV를 지칭하는 AAVhu68.hMfn2 또는 AAVhu68.Mfn2. AAVrh91 캡시드를 갖는 재조합 AAV를 지칭하는 AAVrh91.hMfn2 또는 AAVrh91.Mfn2와 같은 특정 캡시드 유형이 지정될 수 있다.
"재조합 AAV" 또는 "rAAV"는 2개의 요소, AAV 캡시드 및 AAV 캡시드 내에 패키징된 적어도 비-AAV 암호 서열을 함유하는 벡터 게놈을 함유하는 DNAse-내성 바이러스 입자이다. 달리 명시되지 않는 한, 이 용어는 어구 "rAAV 벡터"와 상호교환적으로 사용될 수 있다. rAAV는 임의의 기능성 AAV rep 유전자 또는 기능성 AAV cap 유전자가 결여되어 있고, 자손을 생성할 수 없기 때문에 "복제-결함성 바이러스" 또는 "바이러스 벡터"이다. 특정 구현예에서, 유일한 AAV 서열은 AAV 반전 말단 반복부 서열(ITR)로, 이는 전형적으로 벡터 게놈의 극단 5' 및 3' 단부에 위치하여 ITR 사이에 위치한 유전자 및 조절 서열이 AAV 캡시드 내에 패키징되도록 한다. 일반적으로, AAV 캡시드는 선택된 AAV에 따라 대략 1:1:10 내지 1:1:20의 비율로 20면체 대칭으로 배열된 60개의 캡시드(cap) 단백질 서브유닛, 즉, VP1, VP2, 및 VP3으로 구성된다. 다양한 AAV는 상기 확인된 바와 같이 AAV 바이러스 벡터의 캡시드에 대한 공급원으로 선택될 수 있다. 일 구현예에서, AAV 캡시드는 AAV9 캡시드 또는 이의 조작된 변이체이다. 특정 구현예에서, 변이체 AAV9 캡시드는 AAV9.PhP.eB 캡시드 (서열번호 84의 핵산 서열; 서열번호 85의 아미노산 서열)이다. 특정 구현예에서, PhP.eB 캡시드는 마우스 연구에 사용하기 위해 선택되며, 이는 인간의 클레드(Clade) F 벡터 (예를 들어, AAVhu68)에 적합한 모델이다. 특정 구현예에서, 캡시드 단백질은 rAAV 벡터의 명칭에서 용어 "AAV" 다음에 언급되는 숫자 또는 숫자 및 문자의 조합에 의해 지정된다. 달리 명시되지 않는 한, 본원에 기술된 AAV 캡시드, ITR, 및 다른 선택된 AAV 구성요소는, 제한 없이, AAV1, AAV2, AAV3, AAV4, AAV5, AAV6, AAV7, AAV8, AAV9, AAVrh10, AAVhu37, AAVrh32.33, AAV8bp, AAV7M8 및 AAVAnc80, AAV1, AAV2, AAV3, AAV4, AAV5, AAV6, AAV7, AAV8, AAV9.47, AAV9(hu14), AAV10, AAV11, AAV12, AAVrh8, AAVrh74, AAV-DJ8, AAV-DJ, AAVhu68, 및 AAV9 변이체 (예를 들어, 2020년 12월 1일자로 출원된 미국 가출원 제63/119,863호)로 식별되는 AAV를 포함하되, 제한 없이, 임의의 AAV 중에서 용이하게 선택될 수 있다. 예를 들어, 감소된 캡시드 탈아미드화를 갖는 신규 AAV 벡터 및 이의 용도에 대해 WO 2019/168961호 및 WO 2019/169004호 둘 다; 미국 공개 특허 출원 제2007-0036760-A1호; 미국 공개 특허 출원 제2009-0197338-A1호; EP 제1310571호를 참조한다. 또한, WO 2003/042397호 (AAV7 및 다른 유인원 AAV), 미국 특허 제7790449호 및 미국 특허 제7282199호 (AAV8), WO 2005/033321호 및 US 제7,906,111호 (AAV9), 및 WO 2006/110689호, 및 WO 2003/042397호 (rh.10), WO 2005/033321호, WO 2018/160582호 (AAVhu68)을 참조하고, 이들은 본원에 참조로 포함된다. 또한, WO 2019/168961호 및 WO 2019/169004호를 참조하고, 이들 및 다른 AAV 캡시드에 대한 탈아미드화 프로파일을 기술한다. 다른 적합한 AAV는, 제한 없이, AAVrh90 [2020년 4월 28일자로 출원된 PCT/US20/30273호], AAVrh91 [2020년 4월 28일자로 출원된 PCT/US20/30266호, 및 2020년 11월 4일자로 출원된 미국 특허 가출원 제63/109,734호, 및 2020년 8월 14일자로 출원된 미국 특허 가출원 제63/065,616호] AAVrh92, AAVrh93, AAVrh91.93 [2020년 4월 28일자로 출원된 PCT/US20/30281호]를 포함하고, 이들은 본원에 참조로 포함된다. 다른 적합한 AAV는 2019년 10월 21일자로 출원된 PCT/US20/56511호에 기술된 AAV3B 변이체를 포함하고, AAV3B.AR2.01, AAV3B.AR2.02, AAV3B.AR2.03, AAV3B.AR2.04, AAV3B.AR2.05, AAV3B.AR2.06, AAV3B.AR2.07, AAV3B.AR2.08, AAV3B.AR2.10, AAV3B.AR2.11, AAV3B.AR2.12, AAV3B.AR2.13, AAV3B.AR2.14, AAV3B.AR2.15, AAV3B.AR2.16, 또는 AAV3B.AR2.17을 기술하는 2019년 10월 21일자로 출원된 미국 특허 가출원 제62/924,112호, 및 2020년 5월 15일자로 출원된 미국 특허 가출원 제63/025,753호의 이익을 주장하며, 이들은 본원에 참조로 포함된다. 이들 문헌은 또한 rAAV를 생성하기 위해 선택될 수 있는 다른 AAV 캡시드를 기술하고, 이는 참조로 포함된다. 인간 또는 비-인간 영장류 (NHP)로부터 분리되거나 조작되어 잘 특징지어진 AAV 중에서, 인간 AAV2는 유전자 전달 벡터로 개발된 최초의 AAV이고; 이는 상이한 표적 조직 및 동물 모델에서 효율적인 유전자 전달 실험에 널리 사용되어 왔다.
본원에서 사용된 바와 같이, "벡터 게놈"은 바이러스 입자를 형성하는 파르보바이러스 (예를 들어, rAAV) 캡시드 내부에 패키징된 핵산 서열을 지칭한다. 이러한 핵산 서열은 AAV 반전 말단 반복부 서열(ITR)을 함유한다. 본원의 예에서, 벡터 게놈은 최소한 5'에서 3'으로, AAV 5' ITR, 암호화 서열(들) (즉, 전이유전자(들)), 및 AAV 3' ITR을 함유한다. 캡시드와 상이한 공급원의 AAV인 AAV2 유래의 ITR, 또는 전장 ITR이 아닌 다른 ITR이 선택될 수 있다. 특정 구현예에서, ITR은 생성 동안 rep 기능을 제공하는 AAV 또는 트랜스상보성(transcomplementing) AAV와 동일한 AAV 공급원으로부터 유래된다. 추가로, 다른 ITR, 예를 들어, 자가-상보적 (scAAV) ITR이 사용될 수 있다. 단일 가닥 AAV 및 자가-상보성(sc) AAV 둘 다 rAAV에 포함된다. 전이유전자는 관심이 있는 폴리펩티드, 단백질, 기능성 RNA 분자(예를 들어, miRNA, miRNA 억제제) 또는 다른 유전자 산물을 암호화하는, 벡터 서열에 이종성인 핵산 암호화 서열이다. 핵산 암호화 서열은 표적 조직의 세포에서 전이유전자 전사, 번역 및/또는 발현을 허용하는 방식으로 조절 성분에 작동가능하게 연결된다. 벡터 게놈의 적합한 성분은 본원에 보다 상세하게 논의된다.
일 예에서, "벡터 게놈"은 최소한 5'에서 3'으로, 벡터-특이적 서열, 조작된 인간 Mfn2 암호화 서열을 포함하는 핵산 서열 및 선택적으로 (표적 세포에서 이들의 발현을 지시하는) 조절 제어 서열에 작동가능하게 연결된 내인성 Mfn2를 표적화하는 miRNA 서열을 포함하고, 상기 벡터-특이적 서열은 벡터 게놈을 바이러스 벡터 캡시드 또는 외피 단백질 내로 특이적으로 패키징하는 말단 반복 서열일 수 있다. 예를 들어, AAV 반전 말단 반복부는 AAV 및 다른 특정 파르보바이러스 캡시드 내로 패키징하는 데 이용된다.
특정 구현예에서, 척수강내 주사에 적합한 수성 액체 및 벡터 스톡 (예를 들어, 중추 신경계 및/또는 후근신경절의 세포 (예를 들어, CNS, 예를 들어, 신경 세포(예컨대, 추상세포, 푸르키네 세포, 과립 세포, 방추 세포 및 사이신경세포) 및 아교세포(예컨대, 성상교세포, 희소돌기아교세포, 미세아교세포 및 뇌실막 세포)를 포함함)를 우선적으로 표적화하는 AAV 캡시드를 갖는 rAAV)을 포함하는 조성물이 제공되며, 상기 벡터는 조작된 hMfn2 암호화 서열 및/또는 중추 신경계(CNS)로의 전달을 위한 적어도 하나의 miRNA 특이적 내인성 hMfn2를 갖는다. 특정 구현예에서, 본원에 기술된 바와 같은 하나 이상의 벡터를 포함하는 조성물은 대조(대수조 내)로 후두하 주사를 위해 제형화된다. 특정 구현예에서, 조성물은 컴퓨터 단층촬영-(CT-) rAAV 주사를 통해 투여된다. 특정 구현예에서, 조성물은 오마야 저장소(Ommaya reservoir)를 사용하여 투여된다. 특정 구현예에서, 환자는 조성물의 단일 용량이 투여된다.
본원에서 사용된 바와 같이, "발현 카세트"는 생물학적으로 유용한 핵산 서열 (예를 들어, 단백질, 효소 또는 기타 유용한 유전자 산물, mRNA 등을 암호화하는 유전자 cDNA) 및 상기 핵산 서열 및 이의 유전자 산물의 전사, 번역 및/또는 발현을 지시하거나 조절하는, 이에 작동가능하게 연결된 조절 서열을 포함하는 핵산 분자를 지칭한다. 본원에서 사용된 바와 같이, "작동가능하게 연결된" 서열은 핵산 서열과 인접하거나 비-인접한 조절 서열 및 트랜스 또는 시스 핵산 서열에서 작용하는 조절 서열을 모두 포함한다. 이러한 조절 서열은 전형적으로, 예를 들어, 프로모터, 인핸서, 인트론, 코작 서열, 폴리아데닐화 서열, 및 TATA 신호 중 하나 이상을 포함한다. 발현 카세트는 유전자 서열의 업스트림(5'에서) 조절 서열, 예를 들어, 하나 이상의 프로모터, 인핸서, 인트론 등, 및 하나 이상의 인핸서, 또는 유전자 서열의 다운스트림(3'으로) 조절 서열, 예를 들어, 다른 요소 중에서 폴리아데닐화 부위를 포함하는 3' 비번역 영역(3' UTR)을 함유할 수 있다. 특정 구현예에서, 조절 서열은 유전자 산물의 핵산 서열에 작동가능하게 연결되어 있으며, 상기 조절 서열은 개재 핵산 서열, 즉, 5'-비번역 영역 (5'UTR)에 의해 유전자 산물의 핵산 서열로부터 분리된다. 특정 구현예에서, 발현 카세트는 하나 이상의 유전자 산물의 핵산 서열을 포함한다. 일부 구현예에서, 발현 카세트는 모노시스트로닉 또는 바이시스트로닉 발현 카세트일 수 있다. 다른 구현예에서, 용어 "전이유전자"는 표적 세포 내로 삽입되는 외인성 공급원으로부터의 하나 이상의 DNA 서열을 지칭한다.
전형적으로, 이러한 발현 카세트는 바이러스 벡터를 생성하기 위해 사용될 수 있고, 바이러스 게놈 및 본원에 기술된 것들과 같은 다른 발현 제어 서열의 패키징 신호가 측면에 있는, 본원에 기술된 유전자 산물에 대한 암호화 서열을 함유한다. 특정 구현예에서, 벡터 게놈은 2개 이상의 발현 카세트를 함유할 수 있다.
특정 구현예에서, 발현 카세트는 hMfn2 암호화 서열 (및/또는 내인성 Mfn2를 표적화하는 miRNA 서열), 프로모터를 포함하고, 이에 대한 다른 조절 서열을 포함할 수 있으며, 이 카세트는 벡터(예를 들어, rAAV, 렌티바이러스, 레트로바이러스 등) 내로 패키징될 수 있다.
AAV
재조합 파르보바이러스는 CMT2A의 치료를 위한 벡터로 특히 잘 적합하다. 본원에 기술된 바와 같이, 재조합 파르보바이러스는 AAV 캡시드(또는 보카바이러스 캡시드)를 함유할 수 있다. 특정 구현예에서, 캡시드는 후근신경절 내의 세포 및/또는 하위 운동 뉴런 및/또는 1차 감각 뉴런 내의 세포를 표적화한다. 특정 구현예에서, 본원에서 제공되는 조성물은 내인성 hMfn2 수준을 하향조절하고 hMfn2의 과발현과 관련된 임의의 독성을 감소시키기 위해 조작된 hMfn2 및 내인성 hMfn2를 특이적으로 표적화하는 miRNA를 포함하는 rAAV를 포함하는 단일 rAAV 스톡을 가질 수 있다. 다른 구현예에서, rAAV는 hMfn2를 포함할 수 있고, 내인성 hMfn2를 하향조절하는 miRNA를 포함하는 상이한 벡터와 함께 공동-투여될 수 있다. 다른 구현예에서, rAAV는 내인성 hMfn2를 하향조절하는 적어도 하나의 miRNA를 포함할 수 있고, 제2 벡터 (또는 다른 조성물)는 hMfn2를 전달한다.
예를 들어, 클레드 F (예를 들어, AAVhu68 또는 10 AAV9) 유래 AAV 캡시드를 사용하여 생성된 벡터는 CNS에서 hMfn2를 표적으로 하고 발현하는 벡터를 생성하는 데 사용될 수 있다. 대안적으로, 클레드 A (예를 들어, AAV1, AAVrh91) 유래 AAV 캡시드를 사용하여 생성된 벡터가 선택될 수 있다. 또 다른 구현예에서, 다른 파르보바이러스 또는 다른 AAV 바이러스는 AAV 캡시드의 적합한 공급원일 수 있다.
AAV1 캡시드는 AAV vp1 단백질, AAV vp2 단백질 및 AAV vp3 단백질을 갖는 캡시드를 지칭한다. 특정 구현예에서, AAV1 캡시드는 총 60개의 vp 단백질의 T1 20면체 캡시드 내로 조립된 약 1:1:10의 AAV vp1 단백질, AAV vp2 단백질 및 AAV vp3 단백질의 사전-결정된 비율을 포함한다. AAV1 캡시드는 게놈 서열을 패키징하여 AAV 입자 (예를 들어, 게놈이 벡터 게놈인 재조합 AAV)를 형성할 수 있다. 전형적으로, 가장 긴 vp 단백질, 즉, VP1을 암호화하는 캡시드 핵산 서열은 AAV1 캡시드를 갖는 rAAV의 생성 동안 트랜스로 발현되고, 예를 들어, 미국 특허 제6,759,237호, 미국 특허 제7,105,345호, 미국 특허 제7,186,552호, 미국 특허 제8,637,255호, 및 미국 특허 제9,567,607호에 기술되어 있으며, 이는 본원에 참조로 포함된다. 또한, 참조로 포함된 WO 2018/168961호를 참조한다. 특정 구현예에서, AAV1은 질량 분석법을 사용하여 결정된 바와 같이, 캡시드 내 VP 단백질의 총량을 기준으로, WO 2018/160582호에 정의된 바와 같은 탈아미노화된 VP 이소형의 이종 집단의 캡시드 조성물을 특징으로 하며, 이는 그 전체가 본원에 참조로 포함된다. 특정 구현예에서, AAV 캡시드는 질량 분석법을 사용하여 결정된 바와 같이, 하기 제공된 범위에서 다음 위치 중 하나 이상에서 변형된다. 적합한 변형은 본원에 포함된 탈아미드화의 조절이라고 표지된 상기 단락에 기술된 것들을 포함한다. 특정 구현예에서, 다음의 위치들 중 하나 이상, 또는 N 다음의 글리신은 본원에 기술된 바와 같이 변형된다. 특정 구현예에서, 위치 57, 383, 512 및/또는 718에서 N 다음의 글리신이 보존된 (즉, 변형되지 않은 채로 남아 있는) AAV1 돌연변이가 구성된다. 특정 구현예에서, 선행 문장에서 식별된 4개의 위치에서의 NG는 천연 서열로 보존된다. 특정 구현예에서, 인공 NG는 본원에 참조로 포함된 WO 2018/160582호에서 정의되고 식별된 위치 중 하나와 상이한 위치에 도입된다.
본원에서 사용된 바와 같이, AAVhu68 캡시드는 본원에 참조로 포함된 WO 2018/160582호에 정의된 바와 같은 캡시드를 지칭한다. 본원에 기술된 바와 같이, rAAVhu68은 AAVhu68 핵산으로부터 캡시드를 발현하는 생산 시스템에서 생성된 rAAVhu68 캡시드를 갖는다. 특정 구현예에서, AAVhu68 핵산 서열은 서열번호 81이고, 서열번호 82의 아미노산 서열을 암호화한다. 특정 구현예에서, AAVhu68 핵산 서열은 서열번호 83이고, 서열번호 82의 아미노산 서열을 암호화한다. 단일 핵산 서열 vp1을 사용하여 생성된 rAAVhu68은 vp1 단백질, vp2 단백질 및 vp3 단백질의 이종 집단을 생성한다. 이들 하위집단은 최소한 탈아마이드화된 아스파라긴 (N 또는 Asn) 잔기를 포함한다. 예를 들어, 아스파라긴-글리신 쌍의 아스파라긴은 고도로 탈아마이드화되어 있다. 특정 구현예에서, vp2 및/또는 vp3 단백질은 예를 들어, 선택된 발현 시스템에서 vp 단백질의 비율을 변경하기 위해, vp1과 상이한 핵산 서열로부터 부가적으로 또는 대안적으로 발현될 수 있다.
AAV 캡시드로 패키징되고 숙주 세포에 전달되는 게놈 서열은 전형적으로 최소한 전이유전자 및 이의 조절 서열, 및 AAV 반전 말단 반복부(ITR)로 구성된다. 단일-가닥 AAV 및 자가-상보성(sc) AAV 둘 다 rAAV에 포함된다. 전이유전자는 관심이 있는 폴리펩티드, 단백질, 기능성 RNA 분자(예를 들어, miRNA, miRNA 억제제) 또는 다른 유전자 산물을 암호화하는, 벡터 서열에 이종성인 핵산 암호화 서열이다. 핵산 암호화 서열은 표적 조직의 세포에서 전이유전자 전사, 번역 및/또는 발현을 허용하는 방식으로 조절 성분에 작동가능하게 연결된다.
벡터의 AAV 서열은 전형적으로 시스-작용 5' 및 3' 반전 말단 반복부 서열을 포함한다 (예를 들어, B. J. Carter, in "Handbook of Parvoviruses", ed., P. Tijsser, CRC Press, pp. 155 168 (1990) 참조). ITR 서열은 길이가 약 145 bp이다. 바람직하게는, 실질적으로 ITR을 암호화하는 전체 서열이 분자에 사용되지만, 이들 서열의 약간의 사소한 변형은 허용가능하다. 이들 ITR 서열을 변형시키는 능력은 당업계의 기술 범위 내에 있다. (예를 들어, Sambrook 등, "Molecular Cloning. A Laboratory Manual", 2d ed., Cold Spring Harbor Laboratory, New York (1989); 및 K. Fisher 등, J. Virol., 70:520 532 (1996)과 같은 텍스트 참조). 본 발명에 이용되는 이러한 분자의 예는, 선택된 전이유전자 서열 및 관련 조절 요소에 5' 및 3' AAV ITR 서열이 측면에 있는, 전이유전자를 함유하는 "시스-작용" 플라스미드이다.
ITR은 벡터 생성 동안 게놈의 복제 및 패키징을 담당하는 유전적 요소이며, rAAV를 생성하는 데 필요한 유일한 바이러스 시스 요소이다. 일 구현예에서, ITR은 캡시드를 공급하는 것과 상이한 AAV 유래이다. 바람직한 구현예에서, AAV2 유래의 ITR 서열, 또는 이의 결실된 형태(ΔITR)는 편의를 위해 그리고 규제 승인을 가속화하기 위해 사용될 수 있다. 그러나, 다른 AAV 공급원 유래의 ITR이 선택될 수 있다. ITR의 공급원이 AAV2이고 AAV 캡시드가 또 다른 AAV 공급원 유래인 경우, 생성된 벡터는 위형(pseudotyped)으로 칭해질 수 있다. 전형적으로, AAV 벡터 게놈은 AAV 5' ITR, 유전자 산물(들)을 암호화하는 핵산 서열 및 임의의 조절 서열, 및 AAV 3' ITR을 포함한다. 그러나, 이들 요소의 다른 구성이 적합할 수 있다. 일 구현예에서, 자가-상보적 AAV가 제공된다. D-서열 및 말단 분해 부위(terminal resolution site; trs)가 결실된 ΔITR이라고 하는 5' ITR의 단축 형태가 설명된 바 있다. 특정 구현예에서, 상기 벡터 게놈은 130개 염기쌍의 단축된 AAV2 ITR을 포함하며, 상기 외부 "a" 요소는 결실된다. 단축된 ITR은 내부 A 요소를 주형으로 사용하여 벡터 DNA 증폭 동안 145개 염기쌍의 야생형 길이로 되돌아간다. 다른 구현예에서, 전장 AAV 5' 및 3' ITR이 사용된다.
벡터에 대해 상기 확인된 주요 요소 (예를 들어, rAAV) 외에도, 상기 벡터는 또한 세포에서 이의 전사, 번역 및/또는 발현을 허용하는 방식으로 전이유전자에 작동가능하게 연결된 필수적인 종래의 제어 요소를 포함한다. 본원에서 사용된 바와 같이, 용어 "발현" 또는 "유전자 발현"은 기능성 유전자 산물의 합성에 있어서 유전자로부터의 정보가 사용되는 과정을 지칭한다. 유전자 산물은 단백질, 펩티드 또는 핵산 중합체(예컨대 RNA, DNA 또는 PNA)일 수 있다.
본원에서 사용된 바와 같이, 용어 "조절 서열" 또는 "발현 제어 서열"은 작동가능하게 연결된 단백질을 암호화하는 핵산 서열의 전사를 유도, 억제, 또는 다르게는 제어하는 개시자 서열, 인핸서 서열, 및 프로모터 서열과 같은 핵산 서열을 지칭한다. 조절 제어 요소는 전형적으로 예를 들어, 선택된 5' ITR 서열과 암호화 서열 사이에 위치한, 발현 제어 서열의 일부로서 프로모터 서열을 함유한다. 특히 바람직한 구현예에서, 중추 신경계에 대한 조직 특이적 프로모터가 선택된다. 예를 들어, 프로모터는 신경 세포 프로모터, 예를 들어 gfaABC(1)D 프로모터(Addgene #50473), 또는 인간 Syn 프로모터(서열은 Addgene, Ref. #50465로부터 입수 가능함)일 수 있다.
다른 적합한 프로모터는, 예를 들어, 구성적 프로모터, 조절가능한 프로모터[예를 들어, WO 2011/126808호 및 WO 2013/04943호 참조], 조직 특이적 프로모터, 또는 생리학적 신호에 반응하는 프로모터를 포함할 수 있으며, 이는 사용될 수 있고, 본원에 기술된 벡터에 활용될 수 있다. 프로모터(들)는 상이한 공급원, 예를 들어, 인간 사이토메갈로바이러스(CMV) 급초기 인핸서/프로모터, SV40 초기 인핸서/프로모터, JC 폴리모바이러스 프로모터, 미엘린 염기성 단백질(MBP) 또는 신경교 섬유질 산성 단백질(GFAP) 프로모터, 단순 헤르페스 바이러스(HSV-1) 잠재 연관 프로모터(LAP), 라우스 육종 바이러스(RSV) 긴 말단 반복부(LTR) 프로모터, 뉴런-특이적 프로모터(NSE), 혈소판 유래 성장 인자(PDGF) 프로모터, hSYN, 멜라닌-응집 호르몬(MCH) 프로모터, CBA, 기질 금속단백질 프로모터(MPP), 및 닭 베타-액틴 프로모터로부터 선택될 수 있다. 프로모터 이외에, 벡터는 하나 이상의 다른 적절한 전사 개시, 종결, 인핸서 서열, 효율적인 RNA 처리 신호 예컨대 스플라이싱 및 폴리아데닐화 (폴리A) 신호; 세포질 mRNA 예를 들어 WPRE를 안정화시키는 서열; 번역 효율을 향상시키는 서열(즉, Kozak 공통 서열); 단백질 안정성을 향상시키는 서열; 및 바람직한 경우, 암호화된 산물의 분비를 향상시키는 서열을 함유할 수 있다. 적합한 인핸서의 예는 CMV 인핸서이다. 다른 적합한 인핸서는 목적한 표적 조직 표시에 적합한 것들을 포함한다. 일 구현예에서, 발현 카세트는 하나 이상의 발현 인핸서를 포함한다. 일 구현예에서, 발현 카세트는 2개 이상의 발현 인핸서를 함유한다. 이들 인핸서는 동일할 수 있거나 또는 서로 상이할 수 있다. 예를 들어, 인핸서는 CMV 급초기 인핸서를 포함할 수 있다. 이 인핸서는 서로 인접하게 위치한 2개의 카피에 존재할 수 있다. 대안적으로, 인핸서의 이중 카피는 하나 이상의 서열에 의해 분리될 수 있다. 또 다른 구현예에서, 발현 카세트는 인트론, 예를 들어, 닭 베타-액틴 인트론을 추가로 함유한다. 다른 적합한 인트론은 예를 들어, WO 2011/126808호에 기재된 바와 같이 당업계에 공지된 것들을 포함한다. 적합한 폴리A 서열의 예는 예를 들어, SV40, SV50, 소 성장 호르몬(bGH), 인간 성장 호르몬, 및 합성 폴리A를 포함한다. 특정 구현예에서, 폴리A는 SV40 폴리A이다. 특정 구현예에서, 폴리A는 래빗 글로빈 폴리 A (RBG)이다. 선택적으로, 하나 이상의 서열은 mRNA를 안정화시키기 위해 선택될 수 있다. 이러한 서열의 예는 변형된 WPRE 서열이며, 이는 폴리A 서열의 업스트림 및 암호화 서열의 다운스트림에 조작될 수 있다 [예를 들어, MA Zanta-Boussif 등, Gene Therapy (2009) 16: 605-619 참조].
특정 구현예에서, 벡터 게놈은 조직 특이적 프로모터를 포함한다. 일부 구현예에서, 조직 특이적 프로모터는 인간 시냅신 프로모터이다. 특정 구현예에서, 인간 시냅신 프로모터는 서열번호 6의 핵산 서열을 포함한다. 특정 구현예에서, 벡터 게놈은 구성적 프로모터를 포함하며, 상기 프로모터는 CB7 프로모터 또는 CAG 프로모터이다. 특정 구현예에서, CB7 프로모터는 서열번호 86의 핵산 서열을 포함한다. 특정 구현예에서, CAG 프로모터는 서열번호 87의 핵산 서열을 포함한다.
일 구현예에서, 벡터 게놈은 하기를 포함한다: AAV 5' ITR, 프로모터, 선택적 인핸서, 선택적 인트론, 이를 포함하는 인간 Mfn2 (hMfn2 또는 huMfn2)에 대한 암호화 서열, 폴리 A 및 AAV 3' ITR. 특정 구현예에서, 벡터 게놈은 하기를 포함한다: AAV 5' ITR, 프로모터, 선택적 인핸서, 선택적 인트론, 이를 포함하는 인간 Mfn2에 대한 암호화 서열, 폴리 A 및 AAV 3' ITR. 특정 구현예에서, 벡터 게놈은 하기를 포함한다: AAV 5' ITR, 프로모터, 선택적 인핸서, 선택적 인트론, huMfn2 암호화 서열, 폴리 A 및 AAV 3' ITR. 특정 구현예에서, 벡터 게놈은 하기를 포함한다: AAV2 5' ITR, EF1a 프로모터, 선택적 인핸서, 선택적 프로모터, huMfn2, SV40 폴리 A 및 AAV2 3' ITR. 특정 구현예에서, 벡터 게놈은 AAV2 5' ITR, UbC 프로모터, 선택적 인핸서, 선택적 인트론, huMfn2, SV40 폴리 A 및 AAV2 3' ITR이다. 특정 구현예에서, 벡터 게놈은 AAV2 5' ITR, CB7 프로모터, 인트론, huMfn2, SV40 폴리 A 및 AAV2 3' ITR이다. 특정 구현예에서, 벡터 게놈은 AAV2 5' ITR, CB7 프로모터, 인트론, huMfn2, 래빗 베타 글로빈 폴리 A, 및 AAV2 3' ITR이다. 특정 구현예에서, 벡터 게놈은 AAV2 5' ITR, CB7 프로모터, 인트론, 조작된 huMfn2, 링커, 내인성 huMfn2 서열을 표적으로 하는 miR, 래빗 베타 글로빈 폴리 A, 및 AAV2 3' ITR이다. 특정 구현예에서, 벡터 게놈은 AAV2 5' ITR, CB7 프로모터, 인트론, 조작된 huMfn2, 링커, miR1518 서열, 래빗 베타 글로빈 폴리 A, 및 AAV2 3' ITR이다. 특정 구현예에서, 벡터 게놈은 AAV2 5' ITR, CB7 프로모터, 인트론, 조작된 huMfn2, 링커, miR538, 래빗 베타 글로빈 폴리 A 및 AAV2 3' ITR이다. 예를 들어, 서열번호 1, 3, 69, 71, 73, 75, 77, 및 79를 참조한다. huMfn2 암호화 서열은 본 명세서에서 정의된 것들로부터 선택된다. 예를 들어, 서열번호 11 또는 이와 95% 내지 99.9% 동일한 서열, 또는 서열번호 11 또는 이와 95% 내지 99.9% 동일한 서열, 또는 본원에 정의된 이의 단편을 참조한다. 벡터 게놈의 다른 요소 또는 이들 서열에 대한 변이는 본 발명의 특정 구현예를 위한 벡터 게놈을 위해 선택될 수 있다.
벡터 생성
AAV 바이러스 벡터(예를 들어, 재조합(r) AAV)를 생성하는 데 사용하기 위해, 발현 카세트는 패키징 숙주 세포로 전달되는 임의의 적합한 벡터, 예를 들어 플라스미드로 운반될 수 있다. 본 발명에 유용한 플라스미드는 특히 원핵 세포, 곤충 세포, 포유동물 세포에서 시험관내 복제 및 패키징에 적합하도록 조작될 수 있다. 적합한 형질주입 기법 및 패키징 숙주 세포는 공지되어 있고/있거나 당업계의 기술자에 의해 용이하게 설계될 수 있다.
표 2.
특정 구현예에서, 생성 플라스미드는 캡시드 내로 패키징하기 위한 벡터 게놈을 포함하며, 이는 하기를 포함한다: (a) 인간 미토푸신 2를 암호화하는 조작된 핵산 서열; (b) (a)와 (c) 사이에 위치한 스페이서 서열; (c) (a) 및 (b)의 서열에 대해 3'에 위치한 CMT2 환자의 내인성 인간 미토푸신 2에 특이적인 적어도 하나의 miRNA 서열을 암호화하는 핵산 서열로서; 상기 (a)의 조작된 핵산 서열은 적어도 하나의 miRNA에 대한 표적 부위가 결여되어, miRNA가 조작된 인간 미토푸신 2 암호화 서열을 표적화하는 것을 방지하는, 서열; (c) (a) 및 (c)에 작동가능하게 연결된 조절 서열. 특정 구현예에서, 생성 플라스미드는 서열번호 1, 3, 69, 71, 73, 75, 77, 또는 79의 핵산 서열을 포함하는 벡터 게놈을 포함한다.
벡터로서 사용하기에 적합한 AAV를 생성하고 분리하는 방법은 당업계에 공지되어 있다. 일반적으로, 예를 들어, Grieger & Samulski, 2005, "Adeno-associated virus as a gene therapy vector: Vector development, production and clinical applications," Adv. Biochem. Engin/Biotechnol. 99: 119-145; Buning 등, 2008, "Recent developments in adeno-associated virus vector technology," J. Gene Med. 10:717-733; 및 하기에 인용된 참고문헌을 참조하고, 이들 각각은 그 전체가 본원에 참조로 포함된다. 전이유전자를 비리온 내로 패키징하기 위해, ITR은 발현 카세트를 함유한 핵산 분자와 동일한 작제물에서 시스에 필요한 유일한 AAV 성분이다. cap 및 rep 유전자는 트랜스로 공급될 수 있다.
일 구현예에서, 본원에 기술된 발현 카세트는 바이러스 벡터 생성을 위해 내부에 운반된 면역글로불린 작제물 서열을 패키징 숙주 세포로 전달하는 유전적 요소(예를 들어, 셔틀 플라스미드)로 조작된다. 일 구현예에서, 선택된 유전적 요소는 형질주입, 전기천공, 리포좀 전달, 막 융합 기술, 고속 DNA-코팅 펠릿, 바이러스 감염 및 원형질체 융합을 포함하는 임의의 적합한 방법에 의해 AAV 패키징 세포로 전달될 수 있다. 안정한 AAV 패키징 세포가 또한 제조될 수 있다. 대안적으로, 발현 카세트는 AAV 이외의 바이러스 벡터를 생성하기 위해 또는 시험관 내에서 항체 혼합물의 생성을 위해 사용될 수 있다. 이러한 작제물을 제조하기 위해 사용되는 방법은 핵산 조작의 숙련자에게 알려져 있으며, 유전 공학, 재조합 공학, 및 합성 기술을 포함한다. 예를 들어, Molecular Cloning: A Laboratory Manual, ed. Green and Sambrook, Cold Spring Harbor Press, Cold Spring Harbor, NY (2012)를 참조한다.
용어 "AAV 중간체" 또는 "AAV 벡터 중간체"는 내부에 패키징된 원하는 게놈 서열이 결여된 조립된 rAAV 캡시드를 지칭한다. 이들은 또한 "빈(empty)" 캡시드로 칭해질 수 있다. 이러한 캡시드는 발현 카세트의 검출 가능한 게놈 서열을 함유하지 않거나, 유전자 산물의 발현을 달성하기에 불충분한 부분적으로 패키징된 게놈 서열만을 함유할 수 있다. 이러한 빈 캡시드는 관심 유전자를 숙주 세포로 전달하는 데 비-기능성이다.
본원에 기재된 재조합 아데노-연관 바이러스(AAV)는 알려진 기법을 사용하여 생성될 수 있다. 예를 들어, WO 2003/042397호; WO 2005/033321호, WO 2006/110689호; US 제7588772 B2호를 참조한다. 이러한 방법은 AAV 캡시드 단백질을 암호화하는 핵산 서열; 기능성 rep 유전자; AAV 반전 말단 반복부(ITR) 및 전이유전자가 측면에 있는 본원에 기술된 바와 같은 발현 카세트; 및 AAV 캡시드 단백질로 발현 카세트의 패키징을 허용하기에 충분한 헬퍼 기능을 포함하는 숙주 세포를 배양하는 단계를 수반한다. 또한, AAV 캡시드를 암호화하는 핵산 서열; 기능성 rep 유전자; 기술된 바와 같은 벡터 게놈; 및 AAV 캡시드 단백질로 벡터 게놈의 패키징을 허용하기에 충분한 헬퍼 기능을 함유하는 숙주 세포가 본원에 제공된다. 일 구현예에서, 숙주 세포는 HEK 293 세포이다. 이들 방법은 WO2017160360 A2호에 보다 상세히 기술되어 있으며, 이는 본원에 참조로 포함된다. 캡시드를 생성하는 방법, 이에 대한 암호화 서열, 및 rAAV 바이러스 벡터의 생성 방법이 기술되어 있다. 예를 들어, Gao 등, Proc. Natl. Acad. Sci. U.S.A. 100 (10), 6081-6086 (2003) 및 US 제2013/0045186A1호를 참조한다.
일 구현예에서, 재조합 AAV를 생성하는 데 유용한 생산 세포 배양물이 제공된다. 이러한 세포 배양물은 숙주 세포에서 AAV 캡시드 단백질을 발현하는 핵산; AAV 캡시드로 패키징하기에 적합한 핵산 분자, 예를 들어, 숙주 세포에서 생성물의 발현을 지시하는 서열에 작동가능하게 연결된 유전자 산물을 암호화하는 비-AAV 핵산 서열 및 AAV ITR을 함유하는 벡터 게놈; 및 재조합 AAV 캡시드로 핵산 분자의 패키징을 허용하기에 충분한 AAV rep 기능 및 아데노바이러스 헬퍼 기능을 포함한다. 일 구현예에서, 세포 배양물은 포유동물 세포(예를 들어, 특히 인간 배아 신장 293 세포) 또는 곤충 세포(예를 들어, 바큘로바이러스)로 구성된다.
전형적으로, rep 기능은 벡터 게놈 측면에 있는 ITR을 제공하는 AAV와 동일한 AAV 공급원으로부터 유래된다. 본원에 예에서, AAV2 ITR이 선택되고, AAV2 rep이 사용된다. 선택적으로, 다른 rep 서열 또는 다른 rep 공급원 (및 선택적으로 다른 ITR 공급원)이 선택될 수 있다. 예를 들어, rep은, 이에 제한되지는 않으나, AAV1 rep 단백질, AAV2 rep 단백질; 또는 rep 78, rep 68, rep 52, rep 40, rep68/78 및 rep40/52; 또는 이들의 단편; 또는 또 다른 공급원일 수 있다. 선택적으로, rep 및 cap 서열은 세포 배양물에서 동일한 유전적 요소에 있다. rep 서열과 cap 유전자 사이에 스페이서가 있을 수 있다. 임의의 이들 AAV 또는 돌연변이 AAV 캡시드 서열은 숙주 세포에서 이의 발현을 지시하는 외인성 조절 제어 서열의 제어 하에 있을 수 있다.
일 구현예에서, 세포는 적합한 세포 배양물 (예를 들어, HEK 293) 세포에서 제조된다. 본원에 기술된 유전자 요법 벡터를 제조하는 방법은 당업계에 잘 알려진 방법, 예컨대, 유전자 요법 벡터의 생성에 사용되는 플라스미드 DNA의 생성, 벡터의 생성, 및 벡터의 정제를 포함한다. 일부 구현예에서, 유전자 요법 벡터는 AAV 벡터이고, 생성된 플라스미드는 AAV 게놈 및 관심 유전자를 암호화하는 AAV 시스-플라스미드, AAV rep 및 cap 유전자를 포함하는 AAV 트랜스-플라스미드, 및 아데노바이러스 헬퍼 플라스미드이다. 벡터 생성 과정은, 세포 배양의 개시, 세포 계대, 세포 시딩(seeding), 플라스미드 DNA로 세포의 형질주입, 무혈청 배지로의 형질주입 후 배지 교환, 및 벡터-포함 세포 및 배양 배지의 수확과 같은 방법 단계를 포함할 수 있다.
특정 구현예에서, rAAV.hMfn2에 대한 제조 공정은 플라스미드 DNA를 이용한 HEK293 세포의 일시적 형질주입을 수반한다. 단일 배치(batch) 또는 다중 배치는 PALL iCELLis 바이오리액터에서 HEK293 세포의 PEI-매개 삼중 형질주입에 의해 생성된다. 수확된 AAV 물질은 가능한 경우 일회용 폐쇄 바이오프로세싱 시스템에서 정화, TFF, 친화성 크로마토그래피, 및 음이온 교환 크로마토그래피에 의해 순차적으로 정제된다.
수확된 벡터-함유 세포 및 배양 배지는 본원에서 조(crude) 세포 수확물로 지칭된다. 또 다른 시스템에서, 유전자 요법 벡터는 바큘로바이러스-기반 벡터를 이용하는 감염에 의해 곤충 세포로 도입된다. 이러한 생성 시스템에 대한 검토를 위해, 일반적으로, 예를 들어 Zhang 등, 2009, "Adenovirus-adeno-associated virus hybrid for large-scale recombinant adeno-associated virus production," Human Gene Therapy 20:922-929를 참조하며, 이들 각각의 내용은 그 전체가 본원에 참조로 포함된다. 이들 및 다른 AAV 생성 시스템을 제조하고 사용하는 방법은 또한 하기 미국 특허에 기술되어 있으며, 이들 각각의 내용은 그 전체가 본원에 참조로 포함된다: 제5,139,941호; 제5,741,683호; 제6,057,152호; 제6,204,059호; 제6,268,213호; 제6,491,907호; 제6,660,514호; 제6,951,753호; 제7,094,604호; 제7,172,893호; 제7,201,898호; 제7,229,823호; 및 제7,439,065호이고, 이들은 본원에 참조로 포함된다.
조 세포 수확물은 이후에 추가적인 방법 단계, 예컨대, 벡터 수확물의 농축, 벡터 수확물의 정용여과, 벡터 수확물의 미세유동화, 벡터 수확물의 뉴클레아제 분해, 미세유동화 중간체의 여과, 크로마토그래피에 의한 조 정제, 초원심분리에 의한 조 정제, 접선 흐름 여과에 의한 완충액 교환, 및/또는 벌크 벡터를 제조하기 위한 제형화 및 여과를 거칠 수 있다.
높은 염 농도에서 2 단계 친화성 크로마토그래피 정제 후 음이온 교환 수지 크로마토그래피를 사용하여 벡터 의약품을 정제하고 빈 캡시드를 제거한다. 이러한 방법은 2016년 12월 9일자로 출원된 국제 특허출원 PCT/US2016/065970호에 보다 상세히 기술되어 있으며, 이는 본원에 참조로 포함된다. 2016년 12월 9일자로 출원된 국제 특허출원 PCT/US2016/065976호의 AAV8에 대한 정제 방법, 및 2016년 12월 9일자로 출원된 국제 특허출원 PCT/US16/66013호, 또한 2015년 12월 11일자로 출원된 명칭이 "Scalable Purification Method for AAVrh10"인 rh10에 대한 정제 방법, 및 2016년 12월 9일자로 출원된 국제 특허출원 PCT/US2016/065974호, 2015년 12월 11일자로 출원된 "Scalable Purification Method for AAV1"인 AAV1에 대한 정제 방법은 모두 본원에 참조로 포함된다.
빈 입자 및 전체(full) 입자 함량을 계산하기 위해, 선택된 샘플 (예를 들어, 본원의 예에서 이오딕사놀 구배-정제된 제제, 여기서 GC의 # = 입자의 #)에 대한 VP3 밴드 부피를 로딩된 GC 입자에 대해 표시한다. 생성된 선형 방정식(y = mx+c)을 사용하여 테스트 물품 피크의 밴드 부피에서 입자 수를 계산한다. 이후, 로딩된 20 μL당 입자의 수(pt)에 50을 곱하여 입자(pt)/mL를 제공한다. Pt/mL를 GC/mL로 나눈 값은 게놈 복제물에 대한 입자의 비율(pt/GC)을 제공한다. Pt/mL- GC/mL는 빈 pt/mL를 제공한다. 빈 pt/mL를 pt/mL로 나누고 100을 곱하여 빈 입자의 백분율을 제공한다.
일반적으로, 패키징된 게놈이 있는 AAV 벡터 입자 및 빈 캡시드를 분석하는 방법은 당업계에 공지되어 있다. 예를 들어, Grimm 등, Gene Therapy (1999) 6:1322-1330; Sommer 등, Molec. Ther. (2003) 7:122-128을 참조한다. 변성된 캡시드를 테스트하기 위해, 방법은 처리된 AAV 스톡을, 3가지 캡시드 단백질을 분리할 수 있는 임의의 겔, 예를 들어 완충액에 3-8% 트리스-아세테이트를 포함하는 구배 겔로 이루어진 SDS-폴리아크릴아마이드 겔 전기영동에 적용하는 단계, 그 다음 샘플 물질이 분리될 때까지 겔을 실행하는 단계, 및 겔을 나일론 또는 나이트로셀룰로스 막, 바람직하게는 나일론에 블롯팅하는 단계를 포함한다. 그 다음, 항-AAV 캡시드 항체를 변성 캡시드 단백질에 결합하는 1차 항체, 바람직하게는 항-AAV 캡시드 단클론성 항체, 가장 바람직하게는 B1 항-AAV-2 단클론성 항체로서 사용된다(Wobus 등, J. Virol. (2000) 74:9281-9293). 그 다음, 1차 항체에 결합하고, 1차 항체, 보다 바람직하게는 이에 공유 결합된 검출 분자를 포함하는 항-IgG 항체, 가장 바람직하게는 호스래디쉬 퍼옥시다제에 공유 결합된 양 항-마우스 IgG 항체와의 결합을 검출하기 위한 수단을 포함하는 2차 항체를 사용한다. 결합을 검출하기 위한 방법은 1차 및 2차 항체 사이의 결합을 반-정량적으로 결정하는 데 사용되며, 바람직하게는 방사성 동위원소 방출, 전자기 방사, 또는 비색 변화를 검출할 수 있는 검출 방법, 가장 바람직하게는 화학발광 검출 키트가 사용된다. 예를 들어, SDS-PAGE의 경우, 컬럼 분획으로부터의 샘플을 취하고 환원제(예를 들어, DTT)를 포함하는 SDS-PAGE 로딩 완충액에서 가열될 수 있고, 캡시드 단백질은 미리 주조된 구배 폴리아크릴아마이드 겔(예를 들어, Novex) 상에서 분해되었다. 은 염색은 제조업체의 지침에 따라 SilverXpress(Invitrogen, CA)를 사용하거나 다른 적합한 염색 방법, 즉, SYPRO 루비 또는 쿠마시 염색을 사용하여 수행될 수 있다. 일 구현예에서, 컬럼 분획 중 AAV 벡터 게놈(vg)의 농도는 정량적 실시간 PCR(Q-PCR)에 의해 측정될 수 있다. 샘플을 희석하고 DNase I(또는 또 다른 적합한 뉴클레아제)로 분해하여 외인성 DNA를 제거한다. 뉴클레아제의 비활성화 후, 샘플을 추가로 희석하고, 프라이머 및 프라이머 사이의 DNA 서열에 특이적인 TaqMan™ 형광 프로브를 사용하여 증폭시킨다. 정의된 형광 수준(역치 주기, Ct)에 도달하는 데 필요한 주기 수를 Applied Biosystems Prism 7700 Sequence Detection System에서 각 샘플에 대해 측정한다. AAV 벡터에 포함된 것과 동일한 서열을 포함하는 플라스미드 DNA를 이용하여 Q-PCR 반응에서 표준 곡선을 생성한다. 샘플로부터 얻은 주기 역치(Ct) 값을 사용하여 이를 플라스미드 표준 곡선의 Ct 값으로 정규화함으로써 벡터 게놈 역가를 결정한다. 디지털 PCR에 기반으로 하는 종말점 분석도 또한 사용될 수 있다.
일 측면에서, 광역(broad-spectrum) 세린 프로테아제, 예를 들어 프로테이나제 K(예컨대, Qiagen으로부터 상업적으로 입수 가능함)를 이용하는 최적화된 q-PCR 방법이 사용된다. 보다 구체적으로, 최적화된 qPCR 게놈 역가 분석은, DNase I 분해 후 샘플을 프로테이나제 K로 희석하고 프로테이나제 K로 처리한 다음 열 불활성화시킨다는 점을 제외하고, 표준 분석과 유사하다. 적합하게는 샘플은 샘플 크기와 동일한 양의 프로테이나제 K 완충액으로 희석된다. 프로테이나제 K 완충액은 2배 이상으로 농축될 수 있다. 전형적으로, 프로테아나제 K 처리는 약 0.2 mg/mL이지만, 0.1 mg/mL 내지 약 1 mg/mL로 다양할 수 있다. 처리 단계는 일반적으로 약 55℃에서 약 15분 동안 수행되지만, 더 낮은 온도(예를 들어, 약 37℃ 내지 약 50℃)에서 더 긴 기간(예를 들어, 약 20분 내지 약 30분)에 걸쳐, 또는 더 높은 온도(예를 들어, 최대 약 60℃)에서 더 짧은 기간(예를 들어, 약 5 내지 10분) 동안 수행될 수 있다. 유사하게, 열 불활성화는 일반적으로 약 95℃에서 약 15분 동안이지만, 온도가 더 낮아지고(예를 들어, 약 70 내지 약 90℃) 시간이 연장될 수 있다(예를 들어, 약 20분 내지 약 30분). 그 다음, 샘플을 희석하고(예를 들어, 1000배), 표준 분석에 기술된 바와 같이 TaqMan 분석을 수행한다.
추가적으로, 또는 대안적으로, 액적 디지털 PCR(ddPCR)이 사용될 수 있다. 예를 들어, ddPCR에 의해 단일-가닥 및 자가-상보적 AAV 벡터 게놈 역가를 결정하는 방법이 설명된 바 있다. 예를 들어, M. Lock 등, Hu Gene Therapy Methods. 2014 Apr;25(2):115-25. doi: 10.1089/hgtb.2013.131. Epub 2014 Feb 14를 참조한다.
요약하면, 게놈-결핍 AAV 중간체로부터 패키징된 게놈 서열을 갖는 rAAV 입자를 분리하는 방법은 재조합 AAV 바이러스 입자 및 AAV 캡시드 중간체를 포함하는 현탁액을 고속 성능 액체 크로마토그래피에 적용하는 단계를 수반하며, 상기 AAV 바이러스 입자 및 AAV 중간체는 높은 pH에서 평형화된 강한 음이온 교환 수지에 결합되고, 약 260 및 약 280에서 자외선 흡광도에 대해 용출액을 모니터링하면서 염 구배가 적용된다. pH는 선택된 AAV에 따라 조절될 수 있다. 예를 들어, WO2017/160360호 (AAV9), WO2017/100704호 (AAVrh10), WO 2017/100676호 (예를 들어, AAV8), 및 WO 2017/100674호 (AAV1)를 참조하고, 이는 본원에 참조로 포함된다. 이러한 방법에서, AAV 전체 캡시드는 A260/A280의 비율이 변곡점에 도달할 때 용리되는 분획으로부터 수집된다. 일 예에서, 친화성 크로마토그래피 단계의 경우, 정용여과된 산물은 AAV2 혈청형을 효율적으로 포획하는 Capture Select™ Poros-AAV2/9 친화성 수지(Life Technologies)에 적용될 수 있다. 이러한 이온 조건 하에서, 상당한 백분율의 잔류 세포 DNA 및 단백질이 컬럼을 통해 흐르는 한편, AAV 입자가 효율적으로 포획된다.
비-AAV 및 비-바이러스 벡터
본원에서 사용된 바와 같이, "벡터"는 상기 핵산 서열의 복제 또는 발현을 위해 적절한 표적 세포 내로 도입될 수 있는 핵산 서열을 포함하는 생물학적 또는 화학적 모이어티이다. 벡터의 예는, 이에 제한되지는 않으나, 재조합 바이러스, 플라스미드, 리포플렉스, 폴리머좀, 폴리플렉스, 덴드리머, 세포 투과 펩타이드(CPP) 컨쥬게이트, 자성 입자, 또는 나노입자를 포함한다. 일 구현예에서, 벡터는 이후에 적절한 표적 세포 내로 도입될 수 있는, 외인성 또는 이종성 또는 조작된 hMfn2 암호화 서열 (및/또는 적어도 하나의 miRNA)이 삽입될 수 있는 핵산 분자이다. 이러한 벡터는 바람직하게는 하나 이상의 복제 기점 및 재조합 DNA가 삽입될 수 있는 하나 이상의 부위를 갖는다. 벡터는 종종 벡터를 갖는 세포가 벡터가 없는 세포로부터 선택될 수 있는 수단을 가지며, 예를 들어 벡터는 약물 내성 유전자를 암호화한다. 일반적인 벡터는 플라스미드, 바이러스 게놈, 및 "인공 염색체"를 포함한다. 벡터의 생성, 생산, 특성화, 또는 정량화의 통상적인 방법은 당업계의 기술자에게 이용가능하다.
일 구현예에서, 벡터는 이의 기재된 발현 카세트, 예를 들어, "네이키드 DNA", "네이키드 플라스미드 DNA", RNA, mRNA, shRNA, RNAi 등을 포함하는 비-바이러스 플라스미드이다. 선택적으로, 플라스미드 또는 다른 핵산 서열은 적합한 장치, 예를 들어 전기분무, 전기천공을 통해 전달된다. 다른 구현예에서, 핵산 분자는 예를 들어, 미셀, 리포좀, 양이온성 지질-핵산 조성물, 폴리-글리칸 조성물 및 다른 중합체, 지질 및/또는 콜레스테롤-기반 핵산 컨쥬게이트, 및 본원에 기술된 것과 같은 다른 작제물을 포함하는, 다양한 조성물 및 나노입자와 커플링된다. 예를 들어, WO2014/089486호, US 제2018/0353616A1호, US 제2013/0037977A1호, WO2015/074085A1호, US 제9670152B2호, 및 US 제8,853,377B2호, X. Su 등, Mol. Pharmaceutics, 2011, 8 (3), pp 774-787; web publication: March 21, 2011; WO2013/182683호, WO 2010/053572호 및 WO 2012/170930호를 참조하고, 이들 모두는 본원에 참조로 포함된다.
특정 구현예에서, 비-바이러스 벡터는 공동-투여되는 조작된 hMfn2 서열에 존재하지 않는 부위에서 내인성 hMfn2를 표적화하는 miRNA 전사체의 전달을 위해 사용된다. 일부 구현예에서, miRNA는 용량당 miRNA의 약 0.5 mg/kg 초과 (예를 들어, 약 1.0 mg/kg, 1.5 mg/kg, 2.0 mg/kg, 2.5 mg/kg, 3.0 mg/kg, 4.0 mg/kg, 5.0 mg/kg, 6.0 mg/kg, 7.0 mg/kg, 8.0 mg/kg, 9.0 mg/kg, 또는 10.0 mg/kg 초과) 체중의 양으로 전달된다. 일부 구현예에서, miRNA는 용량당 miRNA의 약 0.1-100 mg/kg (예를 들어, 약 0.1-90 mg/kg, 0.1-80 mg/kg, 0.1-70 mg/kg, 0.1-60 mg/kg, 0.1-50 mg/kg, 0.1-40 mg/kg, 0.1-30 mg/kg, 0.1-20 mg/kg, 0.1-10 mg/kg) 체중 범위의 양으로 전달된다. 일부 구현예에서, miRNA는 용량당 약 1 mg, 5 mg, 10 mg, 15 mg, 20 mg, 25 mg, 30 mg, 35 mg, 40 mg, 45 mg, 50 mg, 55 mg, 60 mg, 65 mg, 70 mg, 75 mg, 80 mg, 85 mg, 90 mg, 95 mg, 100 mg, 150 mg, 200 mg, 250 mg, 300 mg, 350 mg, 400 mg, 450 mg, 또는 500 mg 또는 그 초과의 양으로 전달된다.
특정 구현예에서, miRNA 전사체는 지질 나노입자(LNP)에 캡슐화된다. 본원에서 사용된 바와 같이, 어구 "지질 나노입자"는 하나 이상의 지질 (예를 들어, 양이온성 지질, 비-양이온성 지질, 및 PEG-변형 지질)을 포함하는 전달 비히클을 지칭한다. 바람직하게는, 지질 나노입자는 하나 이상의 miRNA를 하나 이상의 표적 세포(예를 들어, 후근신경절, 하위 운동 뉴런 및/또는 상위 운동 뉴런, 또는 CNS에서 상기 확인된 세포 유형)에 전달하도록 제형화된다. 적합한 지질의 예는 예를 들어, 포스파티딜 화합물 (예를 들어, 포스파티딜글리세롤, 포스파티딜콜린, 포스파티딜세린, 포스파티딜에탄올아민, 스핑고지질, 세레브로시드 및 강글리오시드)을 포함한다. 단독으로 또는 다른 전달 비히클과 조합하여, 중합체를 전달 비히클로 사용하는 것도 고려된다. 적합한 중합체는 예를 들어, 폴리아크릴레이트, 폴리알킬시아노아크릴레이트, 폴리락타이드, 폴리락타이드-폴리글리콜라이드 공중합체, 폴리카프로락톤, 덱스트란, 알부민, 젤라틴, 알지네이트, 콜라겐, 키토산, 사이클로덱스트린, 덴드리머 및 폴리에틸렌이민을 포함할 수 있다. 일 구현예에서, 전달 비히클은 표적 세포로 miRNA의 형질주입을 용이하게 하는 능력을 기반으로 선택된다. miRNA에 유용한 지질 나노입자는 캡슐화하고/하거나 단백질 생산을 위한 데포(depot)로서 역할을 할 표적 세포 내로 miRNA의 전달을 향상시키기 위한 양이온성 지질을 포함한다. 본원에서 사용된 바와 같이, 어구 "양이온성 지질"은 선택된 pH, 예컨대 생리학적 pH에서 순 양전하를 운반하는 임의의 다수의 지질 종을 지칭한다. 상기 고안된 지질 나노입자는 하나 이상의 양이온성 지질, 비-양이온성 지질 및 PEG-변형 지질을 사용하는 다양한 비율의 다성분 지질 혼합물을 포함함으로써 제조될 수 있다. 여러 양이온성 지질이 문헌에 기재되어 있으며, 이들 중 다수는 상업적으로 입수 가능하다. 예를 들어, WO2014/089486호, US 제2018/0353616A1호, 및 US 제8,853,377B2호를 참조하고, 이는 참조로 포함된다. 특정 구현예에서, LNP 제형은 콜레스테롤, 이온화 지질, 헬퍼 지질, PEG-지질 및 캡슐화된 mRNA 주위에 지질 이중층을 형성하는 중합체를 포함하는 정례적인 절차를 사용하여 수행된다(Kowalski 등, 2019, Mol. Ther. 27(4):710-728). 일부 구현예에서, LNP는 헬퍼 지질 DOPE를 갖는 양이온성 지질 (즉, N-[1-(2,3-디올레오일옥시)프로필]-N,N,N-트리메틸암모늄 클로라이드(DOTMA), 또는 1,2-디올레오일-3-트리메틸암모늄-프로판(DOTAP))을 포함한다. 일부 구현예에서, LNP는 이온화 지질 Dlin-MC3-DMA 이온화 지질, 또는 디케토피페라진계 이온화 지질(cKK-E12)을 포함한다. 일부 구현예에서, 중합체는 폴리에틸렌이민(PEI) 또는 폴리(β-아미노)에스테르(PBAE)를 포함한다. 예를 들어, WO2014/089486호, US 제2018/0353616A1호, US 제2013/0037977A1호, WO2015/074085A1호, US 제9670152B2호, 및 US 제8,853,377B2호를 참조하고, 이는 참조로 포함된다.
특정 구현예에서, 본원에 기술된 벡터는 "복제-결함성 바이러스" 또는 "바이러스 벡터"이며, 이는 조작된 hMfn2를 암호화하는 핵산 서열 및/또는 조작된 hMfn2의 서열 상에 존재하지 않는 부위에서 내인성 hMfn2를 표적화하는 적어도 하나의 miRNA를 함유하는 발현 카세트인 합성 또는 인공 바이러스 입자를 지칭한다. 복제-결함성 바이러스는 자손 비리온을 생성할 수 없지만, 표적 세포를 감염시키는 능력을 보유한다. 일 구현예에서, 바이러스 벡터의 게놈은 복제에 필요한 효소를 암호화하는 유전자를 포함하지 않지만 (게놈은 "거트리스(gutless)"로 조작될 수 있음 - 인공 게놈의 증폭 및 패키징에 필요한 신호가 측면에 있는 E2를 암호화하는 핵산 서열만을 함유함), 이러한 유전자는 생성 동안 공급될 수 있다. 따라서, 복제에 필요한 바이러스 효소가 존재하는 경우를 제외하고 자손 비리온에 의한 복제 및 감염이 발생할 수 없기 때문에 유전자 요법에 사용하기에 안전한 것으로 간주된다.
본원에서 사용된 바와 같이, 재조합 바이러스 벡터는 예를 들어, 재조합 아데노-연관 바이러스(AAV), 아데노바이러스, 보카바이러스, 하이브리드 AAV/보카바이러스, 단순 헤르페스 바이러스 또는 렌티바이러스를 포함하는, 임의의 적합한 복제-결함성 바이러스 벡터일 수 있다.
본원에서 사용된 바와 같이, 용어 "숙주 세포"는 벡터(예를 들어, 재조합 AAV)가 생성되는 패키징 세포주를 지칭할 수 있다. 숙주 세포는 임의의 수단, 예를 들어, 전기천공, 인산칼슘 침전, 미세주입, 형질전환, 바이러스 감염, 형질주입, 리포좀 전달, 막 융합 기술, 고속 DNA-코팅 펠릿, 바이러스 감염 및 원형질체 융합에 의해 세포 내로 도입된 외인성 또는 이종성 DNA를 포함하는 원핵 또는 진핵 세포(예를 들어, 인간, 곤충, 또는 효모)일 수 있다. 숙주 세포의 예는, 이에 제한되지는 않으나, 분리된 세포, 세포 배양물, 대장균 세포, 효모 세포, 인간 세포, 비-인간 세포, 포유동물 세포, 비-포유동물 세포, 곤충 세포, HEK-293 세포, 간 세포, 신장 세포, 중추 신경계의 세포, 뉴런, 신경아교세포, 또는 줄기 세포를 포함할 수 있다.
본원에서 사용된 바와 같이, 용어 "표적 세포"는 hMfn2 및/또는 miRNA의 발현이 요구되는 임의의 표적 세포를 지칭한다. 특정 구현예에서, 용어 "표적 세포"는 CMT2A에 대해 치료되는 대상체의 세포를 언급하도록 의도된다. 표적 세포의 예는, 이에 제한되지는 않으나, 중추 신경계 내의 세포를 포함할 수 있다.
조성물
hMfn2.miR (예를 들어, rAAV.hMfn2.miR 스톡)을 포함하는 적어도 하나의 벡터 및/또는 miR을 포함하는 적어도 하나의 벡터 및/또는 스톡을 포함하는 적어도 하나의 벡터, 및 선택적 담체, 부형제 및/또는 보존제를 함유하는 조성물이 본원에 제공된다.
본원에서 사용된 바와 같이, rAAV의 "스톡"은 rAAV의 집단을 지칭한다. 탈아미드화로 인한 캡시드 단백질의 이질성에도 불구하고, 스톡에서 rAAV는 동일한 벡터 게놈을 공유할 것으로 예상된다. 스톡은 예를 들어, 선택된 AAV 캡시드 단백질 및 선택된 생산 시스템의 이종 탈아미드화 패턴 특성이 있는 캡시드를 갖는 rAAV를 포함할 수 있다. 스톡은 단일 생산 시스템에서 생산되거나 생산 시스템의 다중 실행으로부터 풀링될 수 있다. 본원에 기술된 것들을 포함하지만 이에 제한되지 않는 다양한 생산 시스템이 선택될 수 있다.
특정 구현예에서, 조성물은 적어도 CMT2A를 단독으로 또는 다른 벡터 스톡 또는 조성물과 조합하여 치료하는데 사용하기에 적합한 재조합 AAV(rAAV)인 바이러스 스톡을 포함한다. 특정 구현예에서, 상기 조성물은 CMT2A를 치료하기 위한 약제를 제조하는데 사용하기에 적합하다. 특정 구현예에서, 조성물은 CMT2A를 치료하는데 사용하기에 적합한 재조합 AAV(rAAV)인 바이러스 스톡을 포함하며, 상기 rAAV는 하기를 포함한다: (a) 아데노-연관 바이러스 캡시드, 및 (b) AAV 캡시드 내 패키징된 벡터 게놈으로, 상기 벡터 게놈은 AAV 반전 말단 반복부, 조작된 인간 미토푸신 2에 대한 암호화 서열, 스페이서 서열, 조작된 인간 미토푸신 암호화 서열에 존재하지 않는 부위에서 내인성 인간 미토푸신을 특이적으로 표적화하는 적어도 하나의 miRNA에 대한 암호화 서열, 및 암호화된 유전자 산물의 발현을 지시하는 조절 서열을 포함하는, 벡터 게놈. 특정 구현예에서, 조성물은 하기를 포함하는 rAAV를 포함하는 별도의 벡터 스톡을 포함한다: (a) 아데노-연관 바이러스 캡시드, 및 (b) AAV 캡시드 내 패키징된 벡터 게놈으로, 상기 벡터 게놈은 AAV 반전 말단 반복부, 조작된 인간 미토푸신 2에 대한 암호화 서열, 및 암호화된 유전자 산물의 발현을 지시하는 조절 서열을 포함하는, 벡터 게놈 및/또는 (a) 아데노-연관 바이러스 캡시드, 및 (b) AAV 캡시드 내 패키징된 벡터 게놈으로, 상기 벡터 게놈은 AAV 반전 말단 반복부, 조작된 인간 미토푸신 2 암호화 서열에 존재하지 않는 부위에서 내인성 인간 미토푸신 2를 특이적으로 표적화하는 적어도 하나의 miRNA에 대한 암호화 서열, 및 암호화된 유전자 산물의 발현을 지시하는 조절 서열을 포함하는, 벡터 게놈을 포함하는 별도의 벡터 스톡. 특정 구현예에서, 벡터 게놈은 프로모터, 인핸서, 인트론, 인간 Mfn2 암호화 서열 및 폴리아데닐화 신호를 포함한다. 특정 구현예에서, 인트론은 닭 베타 액틴 스플라이스 공여자(splice donor) 및 래빗 β 스플라이스 수용자(splice acceptor) 요소로 구성된다. 특정 구현예에서, 벡터 게놈은 벡터 게놈의 모든 요소의 측면에 있는 AAV2 5' ITR 및 AAV2 3' ITR을 추가로 포함한다.
rAAV.hMfn2.miR (rAAV.hMfn2 또는 다른 벡터)은 인간 CMT2A 환자에게 투여되도록 생리학적으로 양립 가능한 담체에 현탁될 수 있다. 특정 구현예에서, 인간 환자에게 투여하기 위해, 벡터는 식염수, 계면활성제 및 생리학적으로 양립 가능한 염 또는 염의 혼합물을 함유하는 수용액에 적합하게 현탁된다. 적합하게는, 제형은 생리학적으로 허용가능한 pH, 예를 들어, pH 6 내지 9, 또는 pH 6.5 내지 7.5, pH 7.0 내지 7.7, 또는 pH 7.2 내지 7.8의 범위로 조정된다. 척수강내 전달을 위해, 뇌척수액의 pH는 약 7.28 내지 약 7.32, 또는 pH 7.2 내지 7.4이므로, 이 범위 내의 pH가 바람직할 수 있으며; 한편, 정맥내 전달을 위해, 약 6.8 내지 약 7.2의 pH가 바람직할 수 있다. 그러나, 가장 광범위한 범위 내의 다른 pH 및 이러한 하위범위가 다른 전달 경로를 위해 선택될 수 있다.
특정 구현예에서, 제형은 중탄산나트륨을 포함하지 않는 완충 식염수 수용액을 함유할 수 있다. 이러한 제형은 하버드 완충액(Harvard's buffer)과 같은, 물에 인산나트륨, 염화나트륨, 염화칼륨, 염화칼슘, 염화마그네슘 및 이들의 혼합물 중 하나 이상을 포함하는 완충 식염수 수용액을 함유할 수 있다. 수용액은 이전에 상표명 Lutrol® F68로 판매되었던 BASF로부터 상업적으로 입수 가능한 폴록사머인 Kolliphor® P188을 추가로 함유할 수 있다. 수용액은 pH 7.2 또는 pH 7.4일 수 있다.
다른 구현예에서, 제형은 1 mM 인산나트륨(Na3PO4), 150 mM 염화나트륨(NaCl), 3 mM 염화칼륨(KCl), 1.4 mM 염화칼슘(CaCl2), 0.8 mM 염화마그네슘(MgCl2), 및 0.001% Kolliphor® 188을 포함하는 완충 식염수 수용액을 함유할 수 있다. 예를 들어, harvardapparatus.com/harvard-apparatus-perfusion-fluid.html을 참조한다. 특정 구현예에서, 하버드 완충액이 바람직하다.
다른 구현예에서, 제형은 하나 이상의 투과 증진제를 함유할 수 있다. 적합한 투과 증진제의 예는, 예를 들어, 만니톨, 나트륨 글리코콜레이트, 나트륨 타우로콜레이트, 나트륨 데옥시콜레이트, 나트륨 살리실레이트, 나트륨 카프릴레이트, 나트륨 카프레이트, 나트륨 라우릴 설페이트, 폴리옥시에틸렌-9-라우렐 에테르, 또는 EDTA를 포함할 수 있다.
다른 구현예에서, 조성물은 담체, 희석제, 부형제 및/또는 보조제를 포함한다. 적합한 담체는 전달 바이러스가 지시되는 적응증을 고려하여 당업계의 기술자에 의해 용이하게 선택될 수 있다. 예를 들어, 적합한 한 가지 담체는 식염수를 포함하며, 이는 다양한 완충 용액(예를 들어, 인산염 완충 식염수)으로 제형화될 수 있다. 다른 예시적인 담체는 멸균 식염수, 락토스, 수크로스, 인산칼슘, 젤라틴, 덱스트란, 한천, 펙틴, 땅콩유, 참기름, 및 물을 포함한다. 완충액/담체는 rAAV가 주입 튜브에 달라붙는 것을 방지하지만, 생체내에서 rAAV 결합 활성을 방해하지 않는 성분을 포함하여야 한다.
선택적으로, 조성물은, 벡터 (예를 들어, rAAV) 및 담체(들)에 더하여, 다른 통상적인 약제학적 성분, 예컨대, 보존제, 또는 화학적 안정화제를 함유할 수 있다. 적합한 예시적인 보존제는 클로로부탄올, 소르브산칼륨, 소르브산, 이산화황, 프로필 갈레이트, 파라벤, 에틸 바닐린, 글리세린, 페놀, 및 파라클로로페놀을 포함한다. 적합한 화학적 안정화제는 젤라틴 및 알부민을 포함한다.
본원에서 사용된 바와 같이, "담체"는 임의의 및 모든 용매, 분산 매질, 비히클, 코팅제, 희석제, 항균제 및 항진균제, 등장화제 및 흡수 지연제, 완충액, 담체 용액, 현탁액, 콜로이드 등을 포함한다. 약제학적 활성 물질에 대한 이러한 매질 및 작용제의 사용은 당업게에 잘 알려져 있다. 보충 활성 성분이 또한 조성물에 혼입될 수 있다. 어구 "약제학적으로 허용가능한"은 숙주에게 투여될 때 알레르기 반응 또는 유사한 부반응을 일으키지 않는 분자 실체 및 조성물을 지칭한다. 전달 비히클, 예컨대, 리포좀, 나노캡슐, 마이크로입자, 마이크로스피어, 지질 입자, 소포 등이 본 발명의 조성물을 적합한 숙주 세포 내로의 도입을 위해 사용될 수 있다. 특히, rAAV 벡터로 전달되는 전이유전자는 지질 입자, 리포좀, 소포, 나노스피어, 또는 나노입자 등에 캡슐화된 전달을 위해 제형화될 수 있다.
일 구현예에서, 조성물은 대상체에게 전달하기에 적합한 최종 제형을 포함하고, 예를 들어 생리학적으로 양립 가능한 pH 및 염 농도로 완충된 수성 액체 현탁액이다. 선택적으로, 하나 이상의 계면활성제가 제형에 존재한다. 또 다른 구현예에서, 조성물은 대상체에 투여하기 위해 희석되는 농축물로서 수송될 수 있다. 다른 구현예에서, 조성물은 동결건조되고 투여시 재구성될 수 있다.
적합한 계면활성제, 또는 계면활성제의 조합은 무독성인 비이온성 계면활성제 중에서 선택될 수 있다. 일 구현예에서, 예를 들어, 중성 pH를 가지고, 8400의 평균 분자량을 갖는, 폴록사머(Poloxamer) 188로도 알려져있는 Pluronic® F68 [BASF]과 같은 1차 하이드록실기로 종결되는 이작용성 블록 공중합체 계면활성제가 선택된다. 다른 계면활성제 및 다른 폴록사머, 즉, 폴리옥시에틸렌(폴리(에틸렌 옥사이드))의 2개의 친수성 사슬이 측면에 있는 폴리옥시프로필렌(폴리(프로필렌 옥사이드))의 중심 소수성 사슬로 구성된 비이온성 삼중블록 공중합체, SOLUTOL HS 15(마크로골-15 하이드록시스테아레이트), LABRASOL(폴리옥시 카프릴릭 글리세라이드), 폴리옥시 10 올레일 에테르, TWEEN(폴리옥시에틸렌 소르비탄 지방산 에스테르), 에탄올 및 폴리에틸렌 글리콜이 선택될 수 있다. 일 구현예에서, 제형은 폴록사머를 함유한다. 이러한 공중합체는 일반적으로 문자 "P"(폴록사머의 경우)와 그 다음의 세 자리 숫자로 명명되며: 처음 2자리 숫자×100은 폴리옥시프로필렌 코어의 대략적인 분자량을 나타내고, 마지막 숫자×10은 폴리옥시에틸렌 함량 백분율을 나타낸다. 일 구현예에서, 폴록사머 188이 선택된다. 계면활성제는 현탁액의 최대 약 0.0005% 내지 약 0.001%의 양으로 존재할 수 있다.
벡터는 세포를 형질감염시키고 과도한 부작용 없이, 또는 의학적으로 허용가능한 생리학적 효과와 함께 치료적 이익을 제공하는 충분한 수준의 유전자 전달 및 발현을 제공하기에 충분한 양으로 투여되며, 이는 의학 분야의 숙련된 기술자에 의해 결정될 수 있다. 선택적으로, 예를 들어, 목적한 장기(예를 들어, 간(선택적으로 간동맥을 통해), 폐, 심장, 눈, 신장)으로의 직접 전달, 경구, 흡입, 비강내, 기관내, 동맥내, 안내, 정맥내, 근육내, 피하, 피내, 및 다른 비경구 투여 경로와 같은, 척수강내 투여 이외의 경로가 사용될 수 있다. 원하는 경우, 투여 경로는 조합될 수 있다.
벡터의 용량은 주로, 치료될 병태, 환자의 연령, 체중 및 건강과 같은 인자에 따라 달라지고, 이에 따라, 환자에 따라 달라질 수 있다. 예를 들어, 바이러스 벡터의 치료학적으로 효과적인 인간 투여량은 (체중이 70 ㎏인 평균 대상체를 치료하기 위해) 일반적으로 범위 내의 모든 정수 또는 분수 양을 포함하여 약 1 x 109 내지 1 x 1016 게놈 바이러스 벡터의 농도를 함유하는 약 25 내지 약 1000 마이크로리터 내지 약 100 mL의 용액 범위이고, 바람직하게는 인간 환자의 경우 1.0 x 1012 GC 내지 1.0 x 1014 GC이다. 일 구현예에서, 조성물은 범위 내의 모든 정수 또는 분수 양을 포함하여 용량당 적어도 1x109, 2x109, 3x109, 4x109, 5x109, 6x109, 7x109, 8x109, 또는 9x109 GC를 함유하도록 제형화된다. 다른 구현예에서, 조성물은 범위 내의 모든 정수 또는 분수 양을 포함하여 용량당 적어도 1x1010, 2x1010, 3x1010, 4x1010, 5x1010, 6x1010, 7x1010, 8x1010, 또는 9x1010 GC를 함유하도록 제형화된다. 또 다른 구현예에서, 조성물은 범위 내의 모든 정수 또는 분수 양을 포함하여 용량당 적어도 1x1011, 2x1011, 3x1011, 4x1011, 5x1011, 6x1011, 7x1011, 8x1011, 또는 9x1011 GC를 함유하도록 제형화된다. 또 다른 구현예에서, 조성물은 범위 내의 모든 정수 또는 분수 양을 포함하여 용량당 적어도 1x1012, 2x1012, 3x1012, 4x1012, 5x1012, 6x1012, 7x1012, 8x1012, 또는 9x1012 GC를 함유하도록 제형화된다. 또 다른 구현예에서, 조성물은 범위 내의 모든 정수 또는 분수 양을 포함하여 용량당 적어도 1x1013, 2x1013, 3x1013, 4x1013, 5x1013, 6x1013, 7x1013, 8x1013, 또는 9x1013 GC를 함유하도록 제형화된다. 또 다른 구현예에서, 조성물은 범위 내의 모든 정수 또는 분수 양을 포함하여 용량당 적어도 1x1014, 2x1014, 3x1014, 4x1014, 5x1014, 6x1014, 7x1014, 8x1014, 또는 9x1014 GC를 함유하도록 제형화된다. 또 다른 구현예에서, 조성물은 범위 내의 모든 정수 또는 분수 양을 포함하여 용량당 적어도 1x1015, 2x1015, 3x1015, 4x1015, 5x1015, 6x1015, 7x1015, 8x1015, 또는 9x1015 GC를 함유하도록 제형화된다. 일 구현예에서, 인간 적용을 위한 용량은 범위 내의 모든 정수 또는 분수 양을 포함하여 용량당 1x1010 내지 약 1x1012 GC 범위일 수 있다.
특정 구현예에서, 용량은 약 1 x 109 GC/g 뇌 질량 내지 약 1 x 1012 GC/g 뇌 질량의 범위이다. 특정 구현예에서, 용량은 약 1 x 1010 GC/g 뇌 질량 내지 약 3.33 x 1011 GC/g 뇌 질량의 범위이다. 특정 구현예에서, 용량은 약 3.33 x 1011 GC/g 뇌 질량 내지 약 1.1 x 1012 GC/g 뇌 질량의 범위이다. 특정 구현예에서, 용량은 약 1.1 x 1012 GC/g 뇌 질량 내지 약 3.33 x 1013 GC/g 뇌 질량의 범위이다. 특정 구현예에서, 용량은 3.33 x 1011 GC/g 뇌 질량 미만이다. 특정 구현예에서, 용량은 1.1 x 1012 GC/g 뇌 질량 미만이다. 특정 구현예에서, 용량은 3.33 x 1013 GC/g 뇌 질량 미만이다. 특정 구현예에서, 용량은 약 1 x 1010 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 2 x 1010 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 2 x 1010 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 3 x 1010 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 4 x 1010 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 5 x 1010 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 6 x 1010 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 7 x 1010 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 8 x 1010 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 9 x 1010 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 1 x 1011 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 2 x 1011 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 3 x 1011 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 약 4 x 1011 GC/g 뇌 질량이다. 특정 구현예에서, 용량은 rAAV 중 약 1.44 x 1013 내지 4.33 x 1014 GC 범위의 고정 용량(flat dose)으로 인간에게 투여된다. 특정 구현예에서, 용량은 rAAV 중 약 1.44 x 1013 내지 2 x 1014 GC 범위의 고정 용량으로 인간에게 투여된다. 특정 구현예에서, 용량은 rAAV 중 약 3 x 1013 내지 1 x 1014 GC 범위의 고정 용량으로 인간에게 투여된다. 특정 구현예에서, 용량은 rAAV 중 약 5 x 1013 내지 1 x 1014 GC 범위의 고정 용량으로 인간에게 투여된다. 일부 구현예에서, 조성물은 rAAV 중 약 1 x 1013 내지 8 x 1014 GC 범위 내에 있는 AAV의 양을 함유하도록 투여량 단위로 제형화될 수 있다. 일부 구현예에서, 조성물은 rAAV 중 약 1.44 x 1013 내지 4.33 x 1014 GC 범위 내에 있는 rAAV의 양을 함유하도록 투여량 단위로 제형화될 수 있다. 일부 구현예에서, 조성물은 rAAV 중 약 3 x 1013 내지 1 x 1014 GC 범위 내에 있는 rAAV의 양을 함유하도록 투여량 단위로 제형화될 수 있다. 일부 구현예에서, 조성물은 rAAV 중 약 5 x 1013 내지 1 x 1014 GC 범위 내에 있는 rAAV의 양을 함유하도록 투여량 단위로 제형화될 수 있다.
특정 실시양태에서, 벡터는 대상체에게 단일 용량으로 투여된다. 특정 구현예에서, 벡터는 요구되는 다중 주사(예를 들어, 2회 용량)를 통해 전달될 수 있다.
투여량은 임의의 부작용에 대한 치료적 이익의 균형을 맞추도록 조정될 것이며, 이러한 투여량은 재조합 벡터가 사용되는 치료적 적용에 따라 달라질 수 있다. 전이유전자의 발현 수준은 바이러스 벡터, 바람직하게는 미니유전자를 함유하는 AAV 벡터를 생성하는 투여 빈도를 결정하기 위해 모니터링될 수 있다. 선택적으로, 치료 목적을 위해 기술된 것과 유사한 투여 요법이 본원의 조성물을 사용한 면역화에 이용될 수 있다.
본원에서 사용된 바와 같이, 용어 "척수강내 전달" 또는 "척수강내 투여"는 뇌척수액(CSF)에 도달하도록, 척추관, 보다 구체적으로 지주막하 공간으로의 주사를 통한 투여 경로를 지칭한다. 척수강내 전달은 요추 천자, 뇌실내(측뇌실내(ICV)를 포함함), 후두하/수조내, 및/또는 C1-2 천자를 포함할 수 있다. 예를 들어, 물질은 요추 천자를 통해 지주막하 공간 전체에 확산을 위해 도입될 수 있다. 다른 예에서, 주사는 대조 내로 이루어질 수 있다.
본원에서 사용된 바와 같이, 용어 "수조내 전달" 또는 "수조내 투여"는 대조 소뇌연수조(cisterna magna cerebellomedularis)의 뇌척수액으로 직접적으로, 보다 구체적으로 후두하 천자를 통한 또는 대조 내로 직접 주사에 의한 또는 영구적으로 배치된 튜브를 통한 투여 경로를 지칭한다.
(예를 들어, CMT2A 환자에서) 내인성 hMfn2를 억제하기 위해 본원에 기술된 miR 표적 서열을 포함하는 조성물은 일반적으로 뉴런 (예를 들어, 하위 운동 뉴런 및/또는 1차 감각 뉴런을 포함함. 이들은 예를 들어, 추상세포, 푸르키네 세포, 과립 세포, 방추 세포 및 사이신경세포를 포함할 수 있음)을 포함하나, 이에 제한되지 않는 중추 신경계 내의 하나 이상의 상이한 세포 유형을 표적으로 한다.
용도
본원에서 제공되는 벡터 및 조성물은 샤르코-마리-투스(CMT) 장애, 신경병증 또는 이와 관련된 다양한 증상을 가진 환자를 치료하는 데 유용하다. CMT2A를 갖는 환자를 치료하기 위한 병용 요법 또는 공동-요법이 제공된다. 특정 구현예에서, 이러한 요법 또는 공동-요법은 하기를 공동-투여하는 것을 포함한다: (a) 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결된 조작된 인간 미토푸신 2 암호화 서열을 암호화하는 재조합 핵산 서열로서, 상기 인간 미토푸신 2 암호화 서열은 서열번호 15의 서열 또는 이와 적어도 95% 동일한 서열을 갖고, (b)의 miRNA 표적 서열에 미스매치를 가짐에 의해 CMT2A 환자의 내인성 인간 미토푸신 2와 상이한, 재조합 핵산 서열, 및 (b) 인간 CMT2A 대상체의 내인성 인간 미토푸신 2 서열에 특이적인 적어도 하나의 miRNA에 대한 암호화 서열로서, 상기 mRNA는 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되는 것인, 서열.
특정 구현예에서, 이러한 요법 또는 공동-요법은 하기를 공동-투여하는 것을 포함한다: (a) 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결된 조작된 인간 미토푸신 2 암호화 서열을 암호화하는 재조합 핵산 서열로서, 상기 조작된 인간 미토푸신 2 암호화 서열은 서열번호 11의 서열 또는 이와 적어도 95% 동일한 서열을 갖고, (b)의 miRNA 표적 서열에 미스매치를 가짐에 의해 CMT2A 환자의 내인성 인간 미토푸신 2와 상이한, 재조합 핵산 서열, 및 (b) 인간 CMT2A 대상체의 내인성 인간 미토푸신 2 서열에 특이적인 적어도 하나의 miRNA에 대한 암호화 서열로서, 상기 적어도 하나의 miRNA 암호화 서열은 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되고, 상기 적어도 하나의 miRNA 암호화 서열은 서열번호 89 (miR538, 59 nt)를 포함하는 서열을 표적화하는 miRNA 또는 서열번호 27의 안티센스 서열 중 하나 이상을 포함하는 miRNA 중 하나 이상의 서열을 포함하는, 서열.
특정 구현예에서, CMT2A를 갖는 환자를 치료하기 위한 이러한 요법 또는 공동-요법은 하기를 공동-투여하는 것을 포함한다: (a) 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결된 조작된 인간 미토푸신 2 암호화 서열을 암호화하는 재조합 핵산 서열로서, 상기 인간 미토푸신 2 암호화 서열은 (b)의 miRNA 표적 서열에 미스매치를 가짐에 의해 CMT2A 환자의 내인성 인간 미토푸신 2와 상이하도록 조작된 것인, 재조합 핵산 서열, 및 (b) 인간 CMT2A 대상체의 내인성 인간 미토푸신 2 서열에 특이적인 적어도 하나의 miRNA에 대한 암호화 서열로서, 상기 miRNA 암호화 서열은 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되고, 상기 적어도 하나의 miRNA 암호화 서열은 서열번호 15 (miR1693, 64 nt)를 포함하는 miRNA 암호화 서열; 서열번호 15의 적어도 60개의 연속적인 뉴클레오타이드를 포함하는 miRNA 암호화 서열; 서열번호 15와 적어도 99% 동일성을 포함하는 miRNA 암호화 서열로서, 이는 서열번호 15 (또는 서열번호 68)의 약 6개의 뉴클레오타이드 내지 약 26개의 뉴클레오타이드와 100% 동일성을 갖는 서열을 포함하는, miRNA 암호화 서열; 또는 하기 중 하나 이상을 포함하는 miRNA 암호화 서열:
(i) TTGACGTCCAGAACCTGTTCT, 서열번호 27; (ii)
AGAAGTGGGCACTTAGAGTTG, 서열번호 28; (iii)
TTCAGAAGTGGGCACTTAGAG, 서열번호 29; (iv) TTGTCAATCCAGCTGTCCAGC,
서열번호 30; (v) CAAACTTGGTCTTCACTGCAG, 서열번호 31 ; (vi)
AAACCTTGAGGACTACTGGAG, 서열번호 32; (vii)
TAACCATGGAAACCATGAACT, 서열번호 33; (viii)
ACAACAAGAATGCCCATGGAG, 서열번호 34; (ix)
AAAGGTCCCAGACAGTTCCTG, 서열번호 35; (x) TGTTCATGGCGGCAATTTCCT,
서열번호 36; (xi) TGAGGTTGGCTATTGATTGAC, 서열번호 37; (xii)
TTCTCACACAGTCAACACCTT, 서열번호 38; (xiii) TTTCCTCGCAGTAAACCTGCT,
서열번호 39; (xiv) AGAAATGGAACTCAATGTCTT, 서열번호 40; (xv)
TGAACAGGACATCACCTGTGA, 서열번호 41; (xvi)
AATACAAGCAGGTATGTGAAC, 서열번호 42; (xvii)
TAAACCTGCTGCTCCCGAGCC, 서열번호 43; (xviii)
TAGAGGAGGCCATAGAGCCCA, 서열번호 44; (xix)
TCTACCCGCAGGAAGCAATTG, 서열번호 45; 또는 (xx)
CTCCTTAGCAGACACAAAGAA, 서열번호 46, 또는 (i) 내지 (xx) 중 임의의 조합 중 하나 이상의 서열을 갖는, 서열. 특정 구현예에서, 제1 벡터는 핵산 (a)을 포함하고, 제2의 상이한 벡터는 적어도 하나의 miRNA (b)를 포함한다. 특정 구현예에서, 제1 벡터는 바이러스 벡터이고/이거나, 제2 벡터는 바이러스 벡터이고, 제1 및 제2 바이러스 벡터는 동일한 바이러스 공급원 유래일 수 있거나 상이할 수 있다. 특정 구현예에서, 제1 벡터는 비-바이러스 벡터이고, 제2 벡터는 비-바이러스 벡터이고, 제1 및 제2 벡터는 동일한 조성물일 수 있거나 상이할 수 있다.
특정 구현예에서, 본원에 제공되는 벡터 및 조성물은 Mfn2-유도된 지방종증을 갖는 환자를 치료하는데 유용하다. 특정 구현예에서, 본원에 제공되는 벡터 및 조성물은 다발성 대칭성 지방종증을 갖는 환자를 치료하는데 유용하다. 다발성 대칭성 지방종증은 Mfn2 유전자의 희귀한 유전적 돌연변이와 관련이 있고, 상체에 지방 조직이 많이 퇴적되고 축적되는 것을 특징으로 하며, 점차적으로 팔과 다리의 지방 조직이 소실된다(Rocha, N. 등, Human biallelic MFN2 mutations induce mitochondrial dysfunction, upper body adipose hyperplasia, and suppression of leptin expression, eLife, 2017, 6:1-27, April 19, 2017). 특정 구현예에서, 본원에 제공되는 벡터 및 조성물은 Mfn2 결핍으로 인한 중증 조기-발병 신경병증을 갖는 환자를 치료하는데 유용하다. 특정 구현예에서, 본원에 제공되는 벡터 및 조성물은 알츠하이머병(AD), 파킨슨병(PD), 심근병증 및 다양한 암에서 Mfn2-관련 병인을 갖는 환자를 치료하는데 유용하다. Mfn2 조절완화와 AD 및 PD 간의 제안된 연관성, 예를 들어, Mfn2 유전자의 단일 뉴클레오타이드 다형성과 AD 위험 간의 연관성이 있음이 입증되었다(Filadi, R. 등, Cell Death and Disease, 2018, 9:330).
선택적으로, 본원에 제공되는 벡터 및 조성물은 하기로부터 선택되는 하나 이상의 공동-요법과 조합하여 사용될 수 있다: 아세트아미노펜, 비스테로이드성 항염증 약물(NSAID), 삼환계 항우울제 또는 항간질 약물, 예컨대 카르바마제핀 또는 가바펜틴. 또 다른 구현예에서, 벡터는 하나 이상의 스테로이드, 예를 들어 프레드니손을 포함하는 면역조절 요법과 조합하여 전달될 수 있다.
본원에서 사용된 바와 같이, 용어 컴퓨터 단층촬영(CT)은 축을 따라 이루어진 일련의 평면 단면 이미지로부터 컴퓨터에 의해 신체 구조의 3차원 이미지가 구축되는 방사선촬영을 지칭한다.
핵산 또는 이의 단편을 지칭할 때, 용어 "실질적 상동성" 또는 "실질적 유사성"은 다른 핵산 (또는 이의 상보적 가닥)과 적절한 뉴클레오타이드 삽입 또는 결실로 최적으로 정렬되는 경우, 정렬된 서열의 적어도 약 95 내지 99%에서 뉴클레오타이드 서열 동일성이 있음을 나타낸다. 바람직하게는, 상동성은 전장 서열, 또는 이의 오픈 리딩 프레임, 또는 길이가 적어도 15개의 뉴클레오타이드인 또 다른 적합한 단편에 걸쳐 있다. 적합한 단편의 예는 본원에 기술되어 있다.
핵산 서열의 맥락에서, 용어 "서열 동일성" "서열 동일성 퍼센트" 또는 "동일성 퍼센트"는 최대 상응으로 정렬될 때 동일한 2개의 서열에서의 잔기를 지칭한다. 서열 동일성 비교의 길이는 게놈의 전장, 유전자 암호화 서열의 전장에 걸쳐 있을 수 있거나, 또는 적어도 약 500개 내지 5000개의 뉴클레오타이드의 단편이 바람직하다. 그러나, 더 작은 단편 사이의 동일성, 예를 들어, 적어도 약 9개의 뉴클레오타이드, 일반적으로 적어도 약 20개 내지 24개의 뉴클레오타이드, 적어도 약 28개 내지 32개의 뉴클레오타이드, 적어도 약 36개 이상의 뉴클레오타이드의 동일성이 또한 바람직할 수 있다. 유사하게, "서열 동일성 퍼센트"는 단백질의 전장, 또는 이의 단편에 걸쳐 아미노산 서열에 대해 용이하게 결정될 수 있다. 적합하게는, 단편은 적어도 약 8개의 아미노산 길이이며, 최대 약 700개의 아미노산일 수 있다. 적합한 단편의 예는 본원에 기술되어 있다.
용어 "고도로 보존된"은 적어도 80% 동일성, 바람직하게는 적어도 90% 동일성, 그리고 보다 바람직하게는 97% 초과의 동일성을 의미한다. 동일성은 당업계의 기술자에게 알려진 알고리즘 및 컴퓨터 프로그램을 의존함으로써 당업계의 기술자에 의해 용이하게 결정된다.
상한 범위로 달리 명시되지 않는 한, 동일성 백분율은 동일성의 최소 수준이며, 참조 서열에 대해 최대 100% 동일성의 모든 더 높은 수준의 동일성을 포함하는 것으로 이해될 것이다. 달리 명시되지 않는 한, 동일성 백분율은 동일성의 최소 수준이며, 참조 서열에 대해 최대 100% 동일성의 모든 더 높은 수준의 동일성을 포함하는 것으로 이해될 것이다. 예를 들어, "95% 동일성" 및 "적어도 95% 동일성"은 상호교환적으로 사용될 수 있으며, 참조 서열에 대해 95, 96, 97, 98, 99 최대 100% 동일성, 및 이들 사이의 모든 분수를 포함한다.
달리 명시되지 않는 한, 수치는 통상적인 수학적 반올림 규칙을 따르는 것으로 이해될 것이다.
일반적으로, 2개의 상이한 아데노-연관 바이러스 간의 "동일성", "상동성", 또는 "유사성"을 지칭할 때, "동일성", "상동성", 또는 "유사성"은 "정렬된" 서열을 참조하여 결정된다. "정렬된" 서열 또는 "정렬"은, 종종 참조 서열과 비교하여 누락되거나 부가된 염기 또는 아미노산에 대한 보정을 포함하는, 다수의 핵산 서열 또는 단백질(아미노산) 서열을 지칭한다. 예에서, AAV 정렬은 공개된 AAV9 서열을 참조점으로 사용하여 수행된다. 정렬은 공개적으로 또는 상업적으로 이용 가능한 다양한 다중 서열 정렬 프로그램(Multiple Sequence Alignment Programs) 중 임의의 것을 사용하여 수행된다. 이러한 프로그램의 예는 "Clustal Omega", "Clustal W", "CAP Sequence Assembly", "MAP", 및 "MEME"를 포함하며, 이들은 인터넷 웹 서버를 통해 접근 가능하다. 이러한 프로그램에 대한 다른 공급원은 당업자의 기술자에게 알려져 있다. 대안적으로, Vector NTI 유틸리티가 또한 사용된다. 또한, 상기 기술된 프로그램에 함유된 것을 포함하여, 뉴클레오타이드 서열 동일성을 측정하는 데 사용될 수 있는 당업계에 알려진 다수의 알고리즘이 있다. 다른 예에서, 폴리뉴클레오타이드 서열은 GCG 버전 6.1의 프로그램인 Fasta™를 사용하여 비교될 수 있다. Fasta™는 질의 서열과 검색 서열 간에 최상의 중첩 영역의 정렬 및 서열 동일성 퍼센트를 제공한다. 예를 들어, 핵산 서열들 간의 서열 동일성 퍼센트는 본원에 참조로 포함된 GCG 버전 6.1에서 제공되는 바와 같은 디폴트 매개변수(단어 크기 6, 스코어링 매트릭스에 대한 NOPAM 인자)와 함께 Fasta™를 사용하여 결정될 수 있다. 다중 서열 정렬 프로그램, 예를 들어 "Clustal Omega", "Clustal X", "MAP", "PIMA", "MSA", "BLOCKMAKER", "MEME", 및 "Match-Box" 프로그램은 또한 아미노산 서열에 대해 이용 가능하다. 일반적으로, 이들 프로그램 중 임의의 것은 디폴트 설정으로 사용되지만, 당업계의 기술자는 필요에 따라 이러한 설정을 변경할 수 있다. 대안적으로, 당업계의 기술자는 적어도 참조 알고리즘 및 프로그램에 의해 제공되는 바와 같은 동일성 또는 정렬 수준을 제공하는 또 다른 알고리즘 또는 컴퓨터 프로그램을 활용할 수 있다. 예를 들어, J. D. Thomson 등, Nucl. Acids. Res., "A comprehensive comparison of multiple sequence alignments", 27(13):2682-2690 (1999)을 참조한다.
용어 "한(a)" 또는 "하나(an)"는 하나 이상을 지칭한다는 점에 유의해야 한다. 이와 같이, 용어 "한 (또는 "하나", "하나 이상" 및 "적어도 하나"는 본원에서 상호교환적으로 사용된다.
단어 "포함하다", "포함한다", 및 "포함하는"은 배타적이 아니라 포괄적으로 해석되어야 한다. 단어 "이루어지다", "이루어지는", 및 이의 변형은 포괄적이 아니라 배타적으로 해석되어야 한다. 명세서의 다양한 구현예가 "포함하는" 언어를 사용하여 제시되지만, 다른 상황 하에서, 관련 구현예는 또한 "~로 이루어진" 또는 "~로 본질적으로 이루어진" 언어를 사용하여 해석되고 설명되는 것으로 의도된다.
본원에서 사용된 바와 같이, 용어 "약"은 달리 명시되지 않는 한, 주어진 참조값으부터 10%의 가변성(±10%, 예를 들어, ±1, ±2, ±3, ±4, ±5, ±6, ±7, ±8, ±9, ±10 또는 그 사이의 값)을 의미한다.
본원에서 사용된 바와 같이, "질환", "장애" 및 "병태"는 대상체에서 비정상적인 상태를 나타내기 위해 상호교환적으로 사용된다.
본원에서 사용된 바와 같이, 용어 "CMT2A-관련 증상(들)" 또는 "증상(들)"은 CMT2A 환자 뿐만 아니라 CMT2A 동물 모델에서 발견되는 증상(들)을 지칭한다. CMT의 초기 증상에는 하나 이상의 서투름, 발을 들어 올리는데 문제가 있어 보행에 약간의 어려움, 약한 다리 근육, 피로, 반사적 행동의 부재가 포함될 수 있다. CMT2A의 일반적인 증상에는 발 기형(매우 높은 아치형 발/발들), 발목에서 발 들어올림의 어려움(발 떨어짐), 구부러진 발가락(망치족지(hammer toe)로 알려짐), 마른 종아리, 발 또는 손의 무감각 또는 작열감을 초래하는 하퇴부 근육의 소실, 보행시 "부딪힘(Slapping)" (보행시 발이 바닥에 세게 부딪힘), 엉덩이, 다리 또는 발의 약함, 다리 및 손 경련, 균형 소실, 걸려넘어짐(tripping), 및 넘어짐, 물건을 움켜잡고 유지함, 및 항아리와 병 개봉의 어려움, 통증(신경통 및 관절염 통증 모두)이 포함된다. CMT2A의 후기 증상에는 예를 들어, 팔과 손의 유사한 증상, 척추 만곡(척추 측만증)이 포함될 수 있다. CMT2A의 다른 보고된/알려진 증상에는 예를 들어, 발음 및 삼키기 어려움, 특히 평평하게 누워있을 때, 호흡 곤란, 청력 소실, 시력 소실, 성대 마비가 포함될 수 있다.
본원에서 사용된 바와 같이, "환자" 또는 "대상체"는 임상 연구에 사용되는 남성 또는 여성 인간 및 (예를 들어, 개, 비-인간 영장류, 설치류 또는 다른 적합한 모델을 포함하는) 동물 모델을 의미한다. 일 구현예에서, 이들 방법 및 조성물의 대상체는 CMT2A로 진단된 인간이다. 특정 구현예에서, 이들 방법 및 조성물의 인간 대상체는 태아기, 신생아, 유아, 걸음마기 영아(toddler), 취학전 아동, 초등학생, 십대, 청년 또는 성인이다. 추가 구현예에서, 이들 방법 및 조성물의 대상체는 소아 CTM2A 환자이다.
본원에서 사용된 바와 같이, 용어 "치료적 수준"은 건강한 대조군의 적어도 약 5%, 약 8%, 약 10%, 약 15%, 약 20%, 약 25%, 약 30%, 약 35%, 약 40%, 약 45%, 약 50%, 약 55%, 약 60%, 약 65%, 약 70%, 약 75%, 약 80%, 약 85%, 약 90%, 약 95%, 약 100%, 100% 이상, 약 2배, 약 3배 또는 약 5배의 Mfn2 활성을 의미한다. hMfn2의 활성을 측정하기 위한 적합한 분석은 당업계에 공지되어 있다. 일부 구현예에서, 하나 이상의 서브유닛 단백질의 상기 치료적 수준은 CMT2A 관련 증상(들)의 완화; 특정 CMT2A-관련 증상의 역전 및/또는 CMT2A-관련 특정 증상의 진행 방지; 또는 이들의 조합을 초래할 수 있다. 특정 구현예에서, 본원에 제공되는 조성물 및 요법에 의해 전달되는 인간 Mfn2는 기능적 내인성 야생형 단백질의 아미노산 서열을 갖는다. 특정 구현예에서, 상기 서열은 서열번호 19의 아미노산 서열 또는 기능성 인간 Mfn2 단백질과 약 95 내지 100% 동일성인 기능성 단백질이다.
용어 "발현"은 가장 광범위한 의미로 본원에 사용되며, RNA 또는 RNA 및 단백질의 생성을 포함한다. RNA와 관련하여, 용어 "발현" 또는 "번역"은 특히 펩티드 또는 단백질의 생성과 관련된다. 발현은 일시적일 수 있거나 안정적일 수 있다.
추가로 선택적으로, 발현 카세트 (및 벡터 게놈)는 예를 들어, 약물 독성 및/또는 축삭병증을 감소시키기 위해, UTR에 하나 이상의 후근신경절(drg)-miRNA 표적화 서열을 포함할 수 있다. 예를 들어, 모두 명칭이 "Compositions for Drg-Specific Reduction of Transgene Expression"인, 2019년 12월 20일자로 출원된 PCT/US2019/67872호 및 현재 공개된 WO 2020/132455호, 2020년 5월 12일자로 출원된 미국 특허 가출원 제63/023593호, 및 2020년 6월 12일자로 출원된 미국 특허 가출원 제63/038488호를 참조하고, 이는 그 전체가 본원에 포함된다. 일부 구현예에서, 발현 카세트는 유전적 요소(예를 들어, 플라스미드)를 통해 패키징 숙주 세포로 전달되고, 바이러스 벡터(예를 들어, 바이러스 입자)의 캡시드 내로 패키징될 수 있다.
본원에서 사용된 바와 같이, 용어 "작동가능하게 연결된"은 관심 유전자와 인접한 발현 제어 서열 및 관심 유전자를 제어하기 위해 트랜스로 또는 일정 거리에서 작용하는 발현 제어 서열 둘 다를 지칭한다.
단백질 또는 핵산과 관련하여 사용될 때, 용어 "이종"은 단백질 또는 핵산이 자연에서 서로 동일한 관계에서 발견되지 않는 2개 이상의 서열 또는 하위서열을 포함함을 나타낸다. 예를 들어, 새로운 기능성 핵산을 만들기 위해 배열된 관련 없는 유전자로부터의 2개 이상의 서열을 갖는 핵산은 전형적으로 재조합으로 생성된다. 예를 들어, 일 구현예에서, 핵산은 상이한 유전자로부터 암호화 서열의 발현을 지시하도록 배열된 하나의 유전자 유래의 프로모터를 갖는다. 따라서, 암호화 서열과 관련하여, 프로모터는 이종성이다.
본원에 기술된 바와 같이, 조절 요소는 이에 제한되지는 않으나, 하기를 포함한다: 프로모터; 인핸서; 전사 인자;전사 종결자; 효율적인 RNA 처리 신호, 예컨대 스플라이싱 및 폴리아데닐화 신호(폴리A); 세포질 mRNA를 안정화시키는 서열, 예를 들어 우드척 간염 바이러스 (WHP) 전사후 조절 요소 (WPRE); 번역 효율을 향상시키는 서열(즉, 코작 공통 서열).
본 발명의 맥락에서, 용어 "번역"은 리보솜에서의 과정에 관한 것이며, 상기 mRNA 가닥은 아미노산 서열의 조립을 제어하여 단백질 또는 펩티드를 생성한다.
조작된 rMfn2 암호화 서열을 함유하는 발현 카세트, 예를 들어, Syn.PI.hMfn2eng.link.hMfn2.miR1693.WPRE.bGH (서열번호 1의 nt 223 내지 4455); CB7.CI.hMfn2.GA.RBG (서열번호 79의 nt 259 내지 4370); CB7.CI.hMfn2.GA.LINK.miR1518.RBG (서열번호 77의 nt 259 내지 4710); CB7.CI.hMfn2.GA.LINK.miR538.RBG (서열번호 75의 nt 259 내지 4626); CAG.CI.hMfn2.GA.WPRE.SV40 (서열번호 73의 nt 192 내지 4262); CAG.CI.hMfn2.GA.LINK.miR1518.WPRE.SV40 (서열번호 71의 nt 192 내지 4474); 및 CAG.CI.hMfn2.GA.LINK.miR538.WPRE.SV40 (서열번호 69의 nt 192 내지 4474)이 본원에 제공된다.
조작된 rMfn2 암호화 서열을 함유하는 발현 카세트, 예를 들어, Syn.PI.rMnf2eng.link.rMfn2 miR1518 WPRE.BGH (서열번호 3의 nt 223 내지 4430)가 본원에 제공된다.
본 명세서에서 달리 정의되지 않는 한, 본원에서 사용되는 기술적 및 과학적 용어는 당업계의 통상의 기술자에 의해 그리고 공개된 텍스트를 참조하여 일반적으로 이해되는 것과 동일한 의미를 가지며, 이는 본 출원에서 사용되는 다수의 용어에 대한 일반적인 가이드와 함께 당업계의 기술자에게 제공된다.
하기 실시예는 예시일 뿐이며, 본 발명을 제한하는 것으로 의도되지 않는다.
실시예
하기 실시예는 예시이며, 본 발명을 제한하는 것으로 의도되지 않는다.
샤르코-마리-투스 신경병증 제2형A(CMT2A)는 미토콘드리아 융합 및 축삭을 따라 운반하는 데 필요한 단백질인, 미토푸신 2(Mfn2)를 암호화하는 유전자의 돌연변이로 인해 유발된다. 대부분의 경우 CMT2A는 우성-음성 방식으로 작용하는 상염색체 우성 미스센스 돌연변이에 의해 유발된다. 드물게, CMT2A는 열성 기능 상실 돌연변이로 인해 유발된다. Mfn2 돌연변이는 후근신경절(DRG)의 하위 운동 뉴런 및 1차 감각 뉴런에 선택적으로 독성이 있다.
돌연변이 Mfn2의 우성 음성 활성을 극복하기 위해 Mfn2의 과발현에 의해 미토푸신-2 발현을 회복시키는 유전자 요법이 개발되었다. AAV 유전자 요법 기술은 Mfn2 발현 카세트를 뉴런으로 전달하는 데 사용된다. 일부 구현예에서, Mfn2 발현 카세트는 링커를 통해 연결된 miRNA를 포함하고, 상기 miRNA는 돌연변이(결함) Mfn2를 넉다운시켜 돌연변이 Mfn2를 제거하고 정상 미토푸린-2 단백질을 공급하도록 표적화된다. 치료 물품의 주사는 대수조내(ICM)를 통해 또는 정맥내로 전달된다. AAV의 ICM 전달은 하위 운동 뉴런 및 1차 감각 뉴런을 효율적으로 표적화한다. 인간에서의 발현을 위해 고도로 최적화된, 조작된 Mfn2 유전자를 갖는 Mfn2 발현 카세트를 고도로 개선된 중추 신경계(CNS) 형질도입을 갖는 AAV 캡시드와 조합하여 사용하였다.
실시예 1: CMT2A 벡터 전략
AAV 전이유전자 카세트 전략 1에서, 본 발명자들은 프로모터, 인트론, 조작된 Mfn2 cDNA 및 폴리A를 포함하는 Mfn 발현 카세트를 생성하였다. AAV 전이유전자 카세트 전략 2에서, 본 발명자들은 프로모터, 인트론, 발현을 최적화하고 miRNA에 내성이 있도록 조작된, 조작된 Mfn2 cDNA, 내인성 돌연변이 Mfn2를 표적으로 하는 miRNA 및 폴리A를 포함하는 Mfn2 발현 카세트를 생성하였다. 추가로, AAV 전이유전자 카세트 전략 2에서, 생체내에서 miRNA 및 cDNA의 효율적인 발현을 위한 작제물이 확인되었고, 상기 작제물은 시냅신 프로모터, cDNA(조작된 Mfn2), 링커, cDNA의 3' 말단에 위치한 miRNA, WRPE 인핸서 및 폴리A를 포함하였다(데이터는 표시되지 않음).
내인성 Mfn2 유전자를 넉다운시키기 위해, 다양한 miRNA 서열 다양한 miRNA 서열을 조사하였다: miR238, miR1202, miR1518 및 miR2282 등, 표시되지 않은 데이터를 조사하였다. 웨스턴 블롯 분석을 위해, 랫트 B104 세포를 CMV 프로모터, emGFP 전이유전자, miRNA 및 TK 폴리A에 대한 클로닝 부위를 포함하는 시험관내 Block-iT 플라스미드(ThermoFisher)로 형질감염시켰다. Block-iT 온라인 소프트웨어를 사용하여 miRNA를 설계하였다. 세포를 형질감염시키고, 블라스티시딘을 사용하여 발현을 선택하였다. 생존 세포는 대부분 GFP에 대해 양성이었고, 전반적인 형질주입 효율을 결정할 수 있었다. 72시간 후에 B104 세포를 수확하고, 웨스턴 블롯 분석을 위해 준비하였다. 웨스턴 블롯은 Mfn2에 대한 항체 및 로딩 대조군으로서 b-액틴에 대한 항체로 탐침하였다. 도 1a 및 도 1b는 miRNA의 AAV-매개 전달의 정맥내 투여 후 B6 마우스의 마우스 뇌(도 1a) 및 척수(도 1b)에서, qPCR에 의해 측정된, 내인성 Mfn2 RNA의 넉다운을 예시한다. 투여 후 14일째 마우스를 부검한 후, 뇌 및 척수 조직을 수확하고 균질화하였다. 샘플로부터 RNA를 추출하고, Mfn2에 대한 TaqMan 프라이머로 qPCR에 사용하였다. 4개의 처리 그룹을 조사하였다(그룹당 N=5): PBS, AAV9.PHP.eB.CB7.miR_NT(비표적화됨, 3x1011 GC의 용량으로), AAV9.PHP.eB.CB7.miR_1518(3x1011 GC의 용량으로), 및 AAV9.PHP.eB.CB7. miR_1202(3x1011 GC의 용량으로). 조사된 서열 중에서, miR1518은 내인성 Mfn2의 최적의 넉다운을 예시하였다.
도 2a 내지 도 2c는 랫트 Mfn2(rMfn2) cDNA 전이유전자 및 mR1518을 포함하는 AAV 벡터 전달 후 Mfn2 RNA 배수 발현을 예시하며, 상기 AAV 벡터는 마우스에 3x1011 GC의 용량으로 정맥내로 투여되었다. 투여 후 14일째 마우스를 부검한 후, 뇌 및 척수 조직을 수확하고 균질화하였다. 샘플로부터 RNA를 추출하고, Mfn2에 대한 TaqMan 프라이머로 qPCR에 사용하였다. 2개의 처리 그룹을 조사하였다(그룹당 N=5): PBS 및 AAV9.PHP.eB.CB7.miR_1518+rMfn2.
실시예 2: miRNA로 조작된 Mfn2 전이유전자의 발현 카세트를 포함하는 AAV 벡터에 대한 마우스 연구
초기 연구에서, 야생형 마우스에 조작된 랫트 Mfn2(rMfn2) cDNA 핵산 서열(서열번호 12) 및 miRNA1518(서열번호 16)을 포함하는, AAV 벡터를 3x1011 GC로 정맥내로 주사하였다. 4개의 처리 그룹을 조사하였다(각 그룹에서 N=5): PBS, AAV9-PHP.eB.CAG.rMfn2opt.link.rMfn2miR1518.WPRE.SV40, AAV9-PHP.eB.CB7.CI.rMfn2 opt.link.rMfn2miR1518.rBG, 및 AAV9-PHP.eB.hSyn.PI.rMfn2opt.link.rMfn2miR1518.WPRE.bGH (상기 벡터 게놈은 서열번호 3임). 주사 후 14일째에 마우스를 희생시켰다. 뇌 및 척수를 수확하고 균질화하였다. 샘플로부터 RNA를 추출하고, 조작된 랫트 Mfn2 cDNA에 대한 TaqMan 프라이머로 qPCR에 사용하였다. 도 4는 miR1518을 포함하여 조작된 rMfn2 cDNA 전이유전자의 AAV 벡터 전달 후 처리된 마우스의 척수에서 랫트 Mfn2 (rMfn2) cDNA 발현의 배수-발현의 표시된 정량을 예시한다.
추가 조사에서, 야생형 마우스에 조작된 인간 Mfn2(hMfn2) cDNA 핵산 서열(서열번호 11) 및 miRNA1693(서열번호 15)을 포함하는, AAV 벡터를 3x1011 GC로 정맥내로 주사하였다. 4개의 처리 그룹을 조사하였다(각 그룹에서 N=5): PBS, AAV9- PHP.eB.CAG.hMfn2opt.link.hMfn2miR1693.WPRE.SV40, AAV9-PHP.eB.CB7.CI.hMfn2opt.link.hMfn2miR1693.rBG, AAV9- PHP.eB.hSyn.PI.hMfn2opt.link.hMfn2miR1693.WPRE.SV40 (상기 벡터 게놈은 서열번호 1임). 주사 후 14일째에 마우스를 희생시켰다. 뇌 및 척수를 수확하고 균질화하였다. 샘플로부터 RNA를 추출하고, 조작된 인간 Mfn2 cDNA에 대한 TaqMan 프라이머로 qPCR에 사용하였다. 도 5는 miR1693을 포함하여 조작된 hMfn2 cDNA 전이유전자의 AAV 벡터 전달 후 처리된 마우스의 척수에서 인간 Mfn2(hMfn2) cDNA 발현의 배수-발현의 표시된 정량을 예시한다.
인간 및 랫트 Mfn2 발현을 조사한 두 연구에서, 전달된 AAV 벡터 중 CB7, CAG 및 뉴런 특이적 인간 시냅신(hSyn)과 같은 다양한 프로모터를 조사하였다. hSyn 프로모터를 포함하는 AAV 벡터는 척수 조직에서 Mfn2 cDNA의 가장 높은 배수 발현을 나타냈다.
또한, AAV 벡터로부터 처리된 성숙한 miRNA의 총량은 Chen 등, Real-time quantification of micr-RNAs by stem-loop RT-PCR, Nucleic Acid Research, 2005, 33 (20)에 개시된 확립된 절차를 사용하여 조사하였다. 야생형 마우스에 AAV 벡터 또는 대조군 PBS를 3x1011 GC로 정맥내로 주사하였다. 처리 그룹 1의 AAV 게놈 벡터는 miR1693(서열번호 1)을 갖는 hMfn2에 대한 발현 카세트를 포함하며, 이는 링커(서열번호 17)를 통해 miRNA1693(서열번호 15)에 연결된 조작된 인간 Mfn2(hMfn2) cDNA 핵산 서열(서열번호 11)을 추가로 포함한다. 처리 그룹 2의 AAV 벡터는 miR1518(서열번호 3)을 갖는 rMfn2에 대한 발현 카세트를 포함하며, 이는 링커(서열번호 17)를 통해 miRNA1518(서열번호 16)에 연결된 조작된 랫트 Mfn2(rMfn2) cDNA 핵산 서열(서열번호 12)을 추가로 포함한다. 처리 후, 마우스를 주사 후 14일째에 희생시켰다. 뇌 및 척수를 수확하고 균질화하였다. 샘플로부터 RNA를 추출하고, 맞춤형 miRNA 분석에 사용하였다. 맞춤형 miRNA 분석은 cDNA를 생성하고 그 다음 맞춤형 소형 RNA를 생성하기 위한 맞춤형 스템-루프 RT 프라이머: miRNA를 증폭하기 위한 스템 루프 TaqMan 프라이머로 구성된다. 이 분석은 벡터로부터 처리된 성숙한 miRNA의 총량을 측정한다. 도 6a 및 도 6b는 마우스에서 정맥내 전달 후 AAV 벡터로부터 처리된 성숙한 miRNA의 총량을 예시한다.
요약하면, hSyn 프로모터(서열번호 6)는 최대 척수 발현을 위한 최상의 프로모터인 것으로 보인다. "링크"("링커"의 경우)를 포함하는 AAV 벡터는 적절한 miRNA 절제 및 RNAi 처리에 필요한 cDNA와 miRNA 사이의 중요한 스페이서이다. 복제 용이성으로 인해 더 작은 링커를 시도하였지만 작동하지 않았다. qPCR 분석은 내인성 돌연변이 Mfn2를 표적으로 하는 miRNA와 공동-전달될 때 랫트 Mfn2 및 인간 Mfn2의 적절한 발현을 제안한다.
실시예 3. HEK293 및 Mfn2-널 세포에서 AAV 벡터의 형질주입 효율
본 연구에서 본 발명자들은 하기 표 3에 열거된 바와 같이, 조작된 인간 Mfn2 서열의 전이유전자를 포함하는 다양한 AAV 벡터를 생성하고 검사하였다.
표 3.
Mfn2 널 MEF는 Mfn2가 결여된 마우스 세포주로, 이는 벡터에서 Mfn2 cDNA의 발현을 검출하는데 사용되었다. 추가적으로, Mfn 2를 발현하는 인간 세포주인, HEK293 세포는 상기 확인된 벡터를 형질주입시키는데 사용되었다. 형질주입 후, 세포 용해물을 웨스턴 블롯을 통한 전체 Mfn 단백질 발현, qPCR을 통한 내인성 Mfn2 넉다운 및 qPCR을 통한 miRNA의 존재에 대해 분석하였다. 웨스턴 블롯 정량은 Wes 플랫폼으로 수행하였다. Mfn2-널 MEF 세포에서 Mfn 발현의 분석은 세포주가 Mfn2 발현이 결여되어 있기 때문에 벡터에 의해 생산된 Mfn2 단백질만을 정량하였다. qPCR miRNA 검출 분석의 경우, 스템-루프 프라이머를 성숙한 miRNA의 역전사(RT)에 사용하였으며, TaqMan 프로브 세트를 miRNA의 발현 및/또는 처리를 나타내기 위해 성숙한 miRNA의 증폭에 사용하였다. 내인성 인간 Mfn2 넉다운을 측정하기 위한 qPCR의 경우, HEK293 내인성 Mfn2와 벡터 Mfn2를 구별하는 TaqMan 프라이머/프로브 세트를 사용하였다. Wes-기반 Mfn2 단백질 정량의 경우 및 Mfn2에 대한 항체를 사용하였으며, 이는 내인성 및 벡터 생성된 Mfn2와 교차 반응하고, 따라서 전체 Mfn2 과발현을 탐침한다.
도 7은 CB7 프로모터를 포함하는 다양한 벡터로 형질주입 후 Mfn2-널 MEF 세포주에서 Mfn2의 발현 수준을 나타낸다. 또한, 도 7은 CB7.CI.hMfn2.GA.WPRE.RBG (p6165); CB7.CI.hMfn2.GA.LINK.miR1518.RBG (p6166);
CB7.CI.hMfn2.GA.LINK.miR538.RBG (p6167)로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량을 나타낸다. 정량은 발현 퍼센트로 표시되며; 형질주입 효율은 유세포 분석법으로 측정시 약 40%인 것으로 확인되었고, 육안 관찰로 어림잡아 계산되었다. Mfn2의 발현 수준(데이터는 표시되지 않음)에 대해 탐침된 웨스턴 블롯의 경우, b-액틴을 로딩 대조군으로 사용하였다 (Mfn2: 2 μg 로딩됨; b-액틴: 0.27 μg 로딩됨; 정량에 4초 노출 사용됨).
도 8은 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후 Mfn2-널 MEF 세포주에서 Mfn2의 발현 수준을 나타낸다. 또한, 도 8은 CAG.CI.hMfn2.GA.WPRE.SV40 (p6168); CAG.CI.hMfn2.GA.LINK.miR1518.WPRE.SV40 (p6169);
CAG.CI.hMfn2.GA.LINK.miR538.WPRE.SV40 (p6170)로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량을 나타낸다. 정량은 발현 퍼센트로 표시되며; 형질주입 효율은 유세포 분석법으로 측정시 약 40%인 것으로 확인되었고, 육안 관찰로 어림잡아 계산되었다. Mfn2의 발현 수준에 대해 탐침된 웨스턴 블롯의 경우, b-액틴을 로딩 대조군으로 사용하였다 (Mfn2: 2 μg 로딩됨; b-액틴: 0.27 μg 로딩됨; 정량에 4초 노출 사용됨).
도 9a 및 도 9b는 CB7 또는 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후 HEK293 세포주에서 Mfn2의 발현 수준을 나타낸다. 높은 형질주입 효율이 관찰되었다. 도 9a는 CB7 프로모터, (CB7.CI.hMfn2.GA.WPRE.RBG (p6165); CB7.CI.hMfn2.GA.LINK.miR1518.RBG (p6166);
CB7.CI.hMfn2.GA.LINK.miR538.RBG(p6167))를 포함하는 다양한 벡터로 형질주입 후, qPCR에 의해 측정되고 배수 발현으로 표시된 HEK293 세포에서의 내인성 Mfn2 넉다운을 나타낸다. 도 9b는 CAG 프로모터 (CAG.CI.hMfn2.GA.WPRE.SV40 (p6168); CAG.CI.hMfn2.GA.LINK.miR1518.WPRE.SV40 (p6169);
CAG.CI.hMfn2.GA.LINK.miR538.WPRE.SV40 (p6170))을 포함하는 다양한 벡터로 형질주입 후, qPCR에 의해 측정되고 배수 발현으로 표시된 HEK293 세포에서의 내인성 Mfn2 넉다운을 나타낸다.
도 10은 CB7 프로모터를 포함하는 다양한 벡터로 형질주입 후 HEK293 세포주에서 Mfn2 (내인성 Mfn2 및 벡터로부터 발현된 Mfn2)의 발현 수준을 나타낸다. 또한, 도 10은 CB7.CI.hMfn2.GA.WPRE.RBG (p6165);
CB7.CI.hMfn2.GA.LINK.miR1518.RBG (p6166); CB7.CI.hMfn2.GA.LINK.miR538.RBG (p6167)로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량을 나타낸다. 정량은 발현 퍼센트로 표시되며; 형질주입 효율은 약 95%인 것으로 확인되었다. Mfn2의 발현 수준에 대해 탐침된 웨스턴 블롯의 경우, b-액틴을 로딩 대조군으로 사용하였다 (Mfn2: 0.78 μg 로딩됨; b-액틴: 0.78 μg 로딩됨; 정량에 4초 노출 사용됨).
도 11은 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후 HEK293 세포주에서 Mfn2 (내인성 Mfn2 및 벡터로부터 발현된 Mfn2)의 발현 수준을 나타낸다. 또한, 도 11은 CAG.CI.hMfn2.GA.WPRE.SV40 (p6168);
CAG.CI.hMfn2.GA.LINK.miR1518.WPRE.SV40 (p6169);
CAG.CI.hMfn2.GA.LINK.miR538.WPRE.SV40 (p6170)으로 형질주입 후 미토푸린-2 (Mfn2)의 발현을 측정하는 웨스턴 블롯 신호의 표시된 정량을 나타낸다. 정량은 발현 퍼센트로 표시되며; 형질주입 효율은 약 95%인 것으로 확인되었다. Mfn2의 발현 수준에 대해 탐침된 웨스턴 블롯의 경우, b-액틴을 로딩 대조군으로 사용하였다 (Mfn2: 0.78 μg 로딩됨; b-액틴: 0.78 μg 로딩됨; 정량에 4초 노출 사용됨).
도 12a 내지 도 12c는 CB7 또는 CAG 프로모터를 포함하는 다양한 벡터로 형질주입 후, Mfn2-널 MEF 세포주에서 성숙한 miRNA(miR1518 또는 miR538)의 qPCR에 의해 측정된 발현 수준을 나타낸다. 도 12a는 CB7 또는 CAG 프로모터를 포함하는 벡터로 형질주입 후, Mfn2-널 MEF 세포주에서 성숙한 miR1518의 qPCR에 의해 측정되고 배수 발현으로 표시된 발현 수준의 비교를 나타낸다. 도 12b는 CB7 또는 CAG 프로모터를 포함하는 벡터로 형질주입 후, Mfn2-널 MEF 세포주에서 성숙한 miR538의 qPCR에 의해 측정되고 배수 발현으로 표시된 발현 수준의 비교를 나타낸다. 도 12c는 CB7 또는 CAG 프로모터를 포함하는 벡터로 형질주입 후, Mfn2-널 MEF 세포주에서 성숙한 miR1518 및 miR538의 qPCR에 의해 측정되고 배수 발현으로 표시된 발현 수준의 비교를 나타낸다.
실시예 4. 샤르코-마리-투스 질환 제2형A의 모델인, MFN2
R94Q
마우스 (C57BL/6J- Tg(Thy1-MFN2
*
)에서의 효능을 위한 유전자 요법 벡터
7마리의 반접합성 수컷 MFN2R94Q 마우스 (C57BL/6J-Tg(Thy1-MFN2*)44Balo/J, JAX stock# 029745), 2마리의 수컷 C57BL/6J 마우스 (JAX stock# 000664), 및 18마리의 암컷 C57BL/6J 마우스 (JAX stock# 000664)를 바하바(Bar Harbor, ME)의 생체내 연구소로 옮겼다. 마우스는 식별을 위해 귀에 표시를 새겼으며, 유전자형(들)을 확인하였고, HEPA 여과된 공기를 사용하여 개별적으로 그리고 확실하게 환기되는 폴리설포네이트 케이지에 케이지당 3마리의 마우스(수컷 1마리와 암컷 2마리) 밀도로 수용되었다. 동물실은 12시간의 명암 주기(오전 6시 내지 오후 6시 조명)를 제어하는, 인공 형광등으로 전적으로 조명을 비췄다. 동물실의 정상온도 및 상대습도 범위는 각각 22±4℃ 및 50±15%였다. 동물실은 시간당 15회의 공기 교환을 갖도록 설정되었다. pH 2.5 내지 3.0으로 산성화된, 여과된 수돗물 및 정상적인 설치류 사료를 임의로 제공하였다. 마우스는 2번의 번식 라운드에서 10마리의 수컷 C57BL/6J 마우스 및 60마리의 수컷 반접합성 MFN2R94Q 마우스의 연구 코호트를 사육하기 위한 사육자로 사용되었다. P0-P1에서, 총 70마리의 마우스가 연구에 등록되었다.
표 4.
도 13a 내지 도 13f는 마우스 모델의 특성화를 나타낸다. 도 13a는 마우스 유전자형의 도식적 표현을 나타낸다. 도 13b는 웨스턴 블롯팅에 의해 측정된 뇌에서 내인성 및 FLAG-태깅된 MFN2의 상대적인 발현 수준을 특징으로 하는 마우스 표현형 특성화를 나타낸다. 도 13c는 웨스턴 블롯팅에 의해 측정된 척수에서 내인성 및 FLAG-태깅된 MFN2의 상대적인 발현 수준을 특징으로 하는 마우스 표현형 특성화를 나타낸다. 도 13d는 CMT2A 마우스 모델(nTg, MFN2WT, 및 MFN2R49Q)에서 마우스의 측정된 중량(g)을 나타낸다. 도 13e는 낙하에 대한 대기 시간(초)으로 측정된 마우스 표현형 특성화를 나타낸다. 도 13f는 악력(g)에 의해 측정된 마우스 표현형 특성화를 나타낸다.
본 연구에서, 마우스는 상기 표 4에 따라 신생아 ICV 주사에 의해 P0-P1에 투약된다. 마우스의 체중은 매주 측정된다. 15-17주령에, 각 마우스에 대해 하기 테스트가 수행된다: 로타로드 테스트(rotarod test), 악력 테스트, 시력 테스트(안구운동 반응), 선택적 절차. 추가적으로, 복합근활동전위(CMAP) 테스트가 수행된다. 17-19주령에, 마우스를 부검하고 하기 조직을 수집한다: 척수, 경골 신경. 수집된 조직은 EM 고정액으로 고정되고 에폭시 수지에 포매된다. 하나의 절편(section)은 각 조직으로부터 절단된다. 절편은 톨루이딘블루로 염색된다. 염색된 슬라이드가 스캐닝된다. 각 스캐닝된 절편의 경우, 하기 매개변수가 결정된다: 축삭 크기 분포, 축삭 수, 축삭 영역. 그 다음 축삭 영역 분포가 각 그룹에 대해 표시된다.
약리학적 연구에서, 첫 번째 코호트의 경우 그룹당 4-7마리의 마우스를 사용하였다. 연구는 맹검 연구였다. 간략하게, 수컷 MFN2R94W 마우스는 후보 AAVhu68 벡터가 투여된 처리 그룹에서 사용되었다. 신생아 ICV 주사는 투여 경로로 사용되었으며, 7.5x1010 GC AAV 벡터의 3 μL 용량을 양측으로 투여하였다. 체중은 매주 측정되었다. 악력은 6주째에 측정되었다. 도 14a 및 도 14b는 MFN2R94Q 마우스(연구 그룹: G1 - 야생형(WT) 마우스, PBS; G2 - MFN2R94Q 마우스, PBS; G3 - MFN2R94Q 마우스, CB7.MFN2; G4 - MFN2R94Q 마우스, CB7.MFN2.miR1518; G5 - MFN2R94Q 마우스, CB7.MFN2.miR538; G6 - MFN2R94Q 마우스, CAG.MFN2.miR1518; G7 - MFN2R94Q 마우스, CAG.MFN2.miR538)에서 파일럿 약리학적 연구의 결과를 나타낸다. 도 14a는 마우스 그룹 G1 내지 G7에서 측정된 체중 결과((g)으로 표시됨)를 나타낸다. 도 14b는 마우스 그룹 G1 내지 G7에서 측정된 생존 결과(0일 내지 50일에 걸친 생존 확률로 표시됨)를 나타낸다. 도 15는 MFN2R94Q 마우스에서 파일럿 약리학적 연구의 악력 결과((kg)으로 표시됨)를 나타낸다.
실시예 5. 내인성 hMfn2를 표적으로 한 hMfn2 및 miR을 공동-투여하는 AAV 벡터
본 연구에서, AAVhu68.CB7.CI.hMfn2.miR538.RBG
(AAVhu68.CB7.CI.hMfn2.GA.LINK.miR538.RBG로도 지칭됨) 벡터는 뇌척수액(CSF)을 사용하여 단일 주사로 광범위한 분포를 달성하는, 대수조내(ICM) 주사를 통해 레서스 마카크(마카카 물라트타) 또는 시노몰구스 마카크(비인간 영장류(NHP)에 투여된다.
테스트 물품. 본 연구에서는 AAVhu68.CB7.CI.hMfn2.GA.LINK.miR538.RBG를 사용한다. 테스트 물품의 품질 및 순도를 검증하는 분석 인증서가 최종 연구 보고서에 포함될 것이다.
준비. 테스트 물품 희석에 대한 계산은 희석하기 전에 훈련된 GTP 담당자가 수행하고 검증한다. 테스트 물품 희석은 주사 당일 지정된 담당자에 의해 수행된다. 테스트 물품 희석은 추가로 지정된 담당자에 의해 검증된다. 희석된 테스트 물품은 주사 전까지 최대 8시간 동안 젖은 얼음(wet ice) 또는 2-8℃에 보관된다.
보관 샘플. 테스트 및 대조군 물품의 보관 샘플은 지정된 담당자에 의해 유지되고 ≤ -60℃에서 저장한다.
테스트 물품 분석. 지정된 담당자는 테스트 물품이 방출 요구사항을 충족하는지 보장할 책임이 있다. 분석 인증서는 연구 기록에 포함되도록 Vector Core에 의해 제공된다. 모든 결과가 기록된다. 데이터 사본이 연구 노트에 포함되도록 제공된다.
미사용 테스트 물품. NPRP 담당자에게 제공된 사용하지 않은 테스트 물품은 보관을 위해 반환되기 전에 젖은 얼음에 저장된다. 보관 샘플은 ≤ -60℃에서 저장된다.
테스트 시스템. 레서스 마카크(마카카 물라트타) 또는 시노몰구스 마카크가 본 연구에 사용된다.
테스트 시스템 선택의 정당성. 본 연구는 CNS 질환에 대한 miRNA 테스트 물품(벡터)의 대수조내(ICM) 전달을 포함한다. NHP에서 CNS의 크기는 임상 대상 모집단의 대표적인 모델 역할을 한다. 본 연구는 레서스 마카크에 ICM 주사 후 투여-관련 약동학 및 테스트 물품의 안전성의 용량 및 경로에 대한 중요한 데이터를 제공한다. 본 연구에서, 2마리의 동물이 사용된다. NHP는 남성 또는 여성, 4-5세, 및 약 3-10 kg으로부터 선택된다.
순응 기간 및 관리. 격리 및 순응, 동물 사육 및 관리는 표준 운영 절차(SOP) 절차에 따라 수행된다. 마카크는 CTRB의 스테인리스 스틸 케이지에 수용된다. 사육 및 관리는 DVR 담당자에 의해 제공된다.
인증된 영장류 식이 5048 또는 비인간 영장류에 적합한 유사한 식단이 동물 연구에 공급된다. 물은 자동 급수 시스템으로부터 이용가능하며, 모든 마카크가 임의로 접근가능하다. 가능한 개입이 필요한 임의의 병태에 대해 수의사에 의해 마카크가 모니터링된다. 적절한 조치를 결정하기 위해 가능할 때마다 연구 책임자와 상의한다. 그러나, 안락사 가능성을 포함한 긴급 상황에서는 필요에 따라 수의사가 결정을 내리고, 가능한 한 빨리 연구 책임자에게 조언을 받는다. 식품 보상의 형태로 농축, 특정 상호작용 및 조작이 제공된다. 동물은 건물 자동화에 의해 제어되는 12시간의 명암 주기로 유지된다. 목적한 온도 범위는 64-84℉ (18- 29℃)이다. 온도는 가능한 최대 범위까지 이 범위에서 유지된다. 목적한 습도 범위는 30~70%이다. 습도는 가능한 한 최대 범위까지 이 범위에서 유지된다. 각 마카크는 이전에 공급업체가 흉부에 새긴 고유 식별 번호로 식별되었다. 두 동물 모두 단일 처리 그룹에 포함된다.
연구 설계 절차. 두 마리의 레서스 마카크가 본 연구에 사용되었다. 두 마카크 모두 단일 처리 그룹에 포함된다. CSF, CBC, 혈청 화학을 포함하는 기준선 혈액 샘플, 및 기준선 바이오마커 평가는 투약 전 0일에 모든 마카크로부터 수집된다. 바이탈(vital)은 또한 각 마카크로부터 얻는다. 0일째에, 마카크가 진정되고: 테스트 물품 투여 전에 칭량되고 활력 징후가 기록된다.
테스트 물품 투여(AAVhu68.CB7.CI.hMfn2.GA.LINK.miR538.RBG)의 경우, 마카크를 마취하고 SOP에 따라 적절한 진통제를 투여한다. 마카크는 대조 내로 후두하 천자를 통해 테스트 물품을 투여한다. 대수조 내(ICM) 천자 시술의 경우, 마취된 마카크를 동물 보관소에서 시술실로 옮기고, CSF를 수집하고 대조 내로 투여하기 위해 머리를 앞으로 구부린 상태로 측면 와위 자세로 X-레이 테이블에 놓는다. 주사 부위는 무균적으로 준비된다. 무균 기술을 사용하여, CSF의 흐름이 관찰될 때까지 21-27 게이지, 1-1.5 인치 퀸케(Quincke) 척추 바늘(Becton Dickinson)을 후두하 공간으로 전진시킨다. 투약 전에, 1 mL의 CSF가 기준선 분석을 위해 수집된다. 횡단되는 해부학적 구조는 피부, 피하 지방, 경막외 공간, 경질막 및 환추-후두근막을 포함한다. 바늘은 혈액 오염 및 잠재적인 뇌간 손상을 피하기 위해 대조의 더 넓은 위쪽 틈새를 향한다. 바늘 천공의 올바른 배치는 형광 투시경(OEC9800 C-Arm, GE)을 사용하여, 척수조영술을 통해 확인된다. CSF 수집 후, 소구경 T 확장 카테터를 척추 바늘에 연결하여 Iohexol(상표명: Omnipaque 180 mg/mL, General Electric Healthcare) 조영제 및 테스트 물품의 투여를 용이하게 한다. 최대 2 mL의 Iohexol이 카테터와 척추 바늘을 통해 투여된다. CSF 반환을 통해 바늘 위치를 확인하고, 형광투시법으로 바늘을 시각화한 후, 테스트 물품을 포함하는 주사기를 테스트 물품을 포함하는 유연한 링커에 연결하고 대략 2 ml/분의 속도로 주입한다. 투여 후, 바늘을 제거하고 천자 부위에 직접 압력을 가한다. 마카크는 3 x 1013 GC (3.33 x 1011 GC/g 뇌)의 용량으로 테스트 물품(AAVhu68.CB7.CI.hMfn2.GA.LINK.miR538.RBG)의 ICM 투여를 받는다. 마카크 당 주입된 총 부피는 1.0 mL이다. 용량 및 부피는 연구 기록에 문서화되어 있다.
관찰을 위해, 연구 일정(표 5)에 열거된 바와 같이 선택된 시점에서, 마카크(들)는 활력 징후, 임상 병리, 혈청 및 CSF 수집을 포함하지만 이에 제한되지 않는 1일 관찰 이외의 추가 매개변수에 대해 모니터링된다.
채혈을 위해, 하기를 포함하는 일반적인 안전 패널을 위해 말초 정맥으로부터 동물을 채혈한다: AAV에 대한 중화 항체, 혈액학, 임상 화학. 채혈 절차는 SOP에 따라 수행된다. 바이오마커(약력학적 마커)의 변화를 측정하기 위해 추가 혈액 샘플을 수집한다. 전체 혈구 수, 혈청 화학, 바이오마커, AAV에 대한 중화 항체를 위한 채혈 빈도는 연구 프로토콜의 연구 일정 (표 5)에 정의된 바와 같다.
항체 분석(AAV에 대한 중화 항체, 혈청)의 경우, 혈액 샘플(최대 2 mL)을 빨간색 상단 튜브(혈청 분리기 포함 또는 제외)를 통해 수집하고, 응고되도록 한 다음 원심분리한다. 연구 담당자가 혈청을 분리한다. 혈청을 매 항체 시점에 대해 2개의 개별적으로 표시된 마이크로원심분리기 튜브 (연구 번호, 동물 ID, 그룹 번호, 시점, 중화 Ab 및 날짜로 표시됨)에 나누고, ≤ -60℃에서 저장한다.
세포 수 및 감별을 위해, 감별 및 혈소판 수를 포함하는 전체 혈구 수를 위한 혈액 샘플을 표시된 최대 2 mL의 라벤더 탑 튜브 (연구 번호, 동물 ID, 그룹 번호, 시점, CBC 및 수집 날짜)에 수집하고, 4℃에서 저장한다. 혈소판 수 및 감별을 포함한 혈액 세포 수를 위해 혈액(라벤더 상단 튜브에 얼음 팩 포함)을 밤새 Antech Diagnostics, Inc.로 보낸다. 적혈구 수, 헤모글로빈, 헤마토크리트, 혈소판 수, 백혈구 수, 백혈구 감별, 평균적혈구용적(MCV), 평균적혈구혈색소량(MCH), 적혈구 형태에 대해 하기 매개변수를 분석한다.
임상 화학의 경우, 혈액 샘플(최대 2 mL)을 표시된 빨간색 상단 튜브에 수집하고 응고되도록 한 다음 원심분리한다. 혈청을 분리하고, 라벨이 부착된 마이크로원심분리기 튜브(연구 번호, 동물 ID, 그룹 번호, 시점, 화학 및 수집 날짜)에 넣고, 분석을 위해 얼음 팩에서 밤새 Antech Diagnostics, Inc.로 보낸다. 하기 매개변수가 분석된다: 알칼리성 포스파타아제, 빌리루빈(총), 크레아티닌, 감마-글루타밀 트랜스펩티다아제, 글루코오스, 혈청 알라닌 아미노전이효소, 혈청 아스파테이트 아미노전이효소, 알부민, 알부민/글로불린 비율(계산됨), 알돌라아제, 혈액 요소 질소, 칼슘, 클로라이드, 크레아티닌 키나아제 및 이소형, 글로불린(총 단백질 - 알부민= 글로불린으로 계산됨), 젖산 탈수소효소, 인, 무기물, 칼륨, 나트륨, 총 단백질.
바이오마커 분석을 위해, 혈액 샘플 (최대 2 mL)을 빨간색 상단 튜브(혈청 분리기 포함 또는 제외)를 통해 수집하고 응고되도록 한 다음 원심분리한다. 연구 담당자가 혈청을 분리한다. 그런 다음 혈청을 2개의 개별적으로 표시된 마이크로원심분리기 튜브 (연구 번호, 동물 ID, 그룹 번호, 시점, 혈청 바이오마커 및 수집 날짜)로 나눈다. 샘플은 ≤ -60℃에서 저장된다.
PBMC/조직 림프구 분리 및 ELISPOT의 경우, 혈액 샘플(6-10 mL)을 나트륨 헤파린(녹색 상단 튜브)에 수집하고, PBMC를 SOP에 따라 분리한다. 혈액 수집 튜브에는 연구 번호, 동물 ID, 그룹 번호, 종, 시점, PBMC 및 수집 날짜가 표시되어 있다. 림프구는 SOP에 따라 비장, 간 및 골수로부터 수확된다. 캡시드 및 전이유전자 T 세포 반응에 대한 ELISPOT은 SOP에 따라 수행된다.
CSF 수집의 경우, 분석 및 바이오마커 평가를 위해 최대 1 mL의 CSF가 수집된다. 연구 0일을 포함하는 모든 CSF 수집 시점에 대해, 마카크는 SOP에 따라 마취하고, 동물 보관소에서 시술실로 옮기고, CSF 수집을 위해 머리를 앞으로 구부린 상태로 측면 와위 자세로 놓는다. 후두부와 경추 상부의 모발을 잘라낸다. 두개골의 후두부 돌기와 환추 날개(C1)를 손으로 만져 검진한다. 주사 부위는 무균적으로 준비된다. 무균 기술을 사용하여, CSF의 흐름이 관찰될 때까지 21-27 게이지, 1-1.5 인치 퀸케 척추 바늘(BD) 또는 21-27 게이지 바늘을 수조로 전진시킨다. 횡단되는 해부학적 구조는 피부, 피하 지방, 경막외 공간, 경질막 및 환추-후두근막을 포함한다. 바늘은 혈액 오염 및 잠재적인 뇌간 손상을 피하기 위해 대조의 더 넓은 위쪽 틈새를 향한다. CSF 수집 후, 바늘을 제거하고 천자 부위에 직접 압력을 가한다. 샘플은 연구 번호, 동물 ID, 그룹 번호, 시점, CSF 및 수집 날짜가 표시된 멸균 1.5 mL Eppendorf 튜브에 수집된다. 샘플을 젖은 얼음 위에 놓고, CSF 임상 병리학(혈액 세포 계수 및 감별 및 총 단백질 정량) 및 CSF 바이오마커를 위해 즉시 분주한다. CSF는 연구 프로토콜의 연구 일정(표 5)에 요약된 빈도로 수집된다.
CSF 임상 병리학의 경우, CSF (0.5 mL)를 혈액 세포 계수 및 감별 및 총 단백질 정량을 위해 라벤더 탑 튜브(연구 번호, 동물 ID, 그룹 번호, 시점, CSF 임상 병리, 및 얼음 팩 날짜로 표시됨)에 분주한다.
CSF 바이오마커의 경우, 멸균된 1.5 mL Eppendorf 튜브 2개에 수집된 나머지 모든 CSF (CSF 임상 병리에 사용되지 않음 - 최대 1 mL)는 800 g에서 5분 동안 원심분리된다. 연구 담당자는 상층액을 분리하고 초저온 바이알(cryovial)에 분주한다 (연구 번호, 동물 ID, 그룹 번호, 시점, CSF 바이오마커 및 수집 날짜로 표시됨). 샘플은 젖은 얼음으로 발송한다.
추가적으로, 모니터링을 위해 선택된 모든 날에 각 마카크를 진정시키고, 칭량하였으며, 임의의 혈액 샘플을 채취하기 전에 호흡 및 심박수를 모니터링하고, 직장 온도계를 통해 체온을 측정하였다. PBMC 분리를 위한 혈액 샘플은 실온에서 수송된다. 다른 샘플은 젖은 얼음으로 수송된다.
본 연구는 하기 표 5에 기술된 바와 같은 일정에 따라 수행된다.
표 5.
마카크를 부검하는 경우, 하기 표 6에 기술된 조직을 수집한다.
표 6. 조직병리학 및 생체내 분포를 위해 부검시에 수집되는 조직
√= 표시된 분석을 위해 조직이 수집되고 처리될 것이다, Req. = 프로토콜에 의해 요구됨, Coll. = 수집됨, N/A = 해당 없음
약어: L, 좌측; R, 우측
A. 뇌 전체를 수집한 다음 정중면을 따라 반으로 나눈다. 뇌의 전체 우측 절반은 조직병리학을 위해 10% 중성 완충 포르말린에 배치되고, "Pardo 등, 2012, Technical Guide for Nervous System Sampling of the Cynomolgus Monkey for General Toxicity Studies, Toxicologic Pathology 40: 624-636"에 따라 추가로 트리밍되고(trimmed) 처리된다. 생체내 분포를 위한 샘플은 좌측 반구로부터 수집되고 ≤ -60℃에서 저장된다.
B. 최소 3개의 경추, 3개의 흉추 및 3개의 요추 후근신경절을 샘플링하고, 조직병리학을 위해 3개의 조직 카세트(경추, 흉추, 요추) 내에 고정한다. 또한, 3개의 반대측 경추 후근신경절, 3개의 반대측 흉추 후근신경절 및 3개의 반대측 3개의 요추 후근신경절을 샘플링하고, 생체내 분포를 위해 ≤-60℃로 동결된다.
C. 심장 절편은 우심실 및 좌심실(AV 판막 포함)과 심실중격(판막 포함)이 포함되어야 한다.
D. 각 척수는 각각 C, T 또는 L로 표시된 경추, 흉추 및 요추 분절로 나뉜다. 각 척수 분절은 세 부분으로 나뉜다. 3개의 C, T 또는 L 섹션은 각각 1-3으로 번호가 매겨질 것이다. 각 동물로부터, C1-3, T1-3 및 L1-3으로 번호가 매겨진 총 9개의 척수 섹션이 생성된다. 각 척수 분절로부터, 섹션 1(C1, T1, L1)은 조직병리학적 분석에 사용된다. 각 척수 분절로부터, 섹션 2(C2, T2, L2)는 생체내 분포 분석(RNA 및 단백질 분석, 2개의 튜브)에 사용된다. 각 척수 분절로부터, 섹션 3(C3, T3, L3)은 LCM에 대해 포르말린 고정되고 파라핀 포매된다.
E. 삼차 신경의 일부는 가능한 직업과 관련된 건강 노출을 위해 수집되고 ≤-60℃에 보관된다.
F. 조직병리학이 적절하지 않은 부검시 이루어진 총체적 관찰(예를 들어, 체액, 헝클어진 모발, 결실된 해부학적 부분)이 수집된다.
실험적 평가: 관찰
생존가능성 확인(케이지내(In-Cage))을 위해, 마카크는 일반적인 외관, 독성 징후에 대해 매일 육안 관찰로 모니터링되며, 이는 이에 제한되지는 않으나, 신경학적 징후 또는 무기력, 고통 및 행동 변화가 포함될 수 있다. 이는 SOP에 따라 담당자에 의해 수행된다. 수의사 및 연구 책임자는 임의의 비정상적인 병태에 대해 통지받는다. 마카크를 위태롭게 하는 긴급 상황이나 보조 수의사 및 연구 책임자에게 적시에 연락할 수 없는 경우 마카크를 인도적으로 희생시키는 경우를 제외하고, 치료는 수의사 및 연구 책임자의 승인 후에만 수행된다.
죽은 채로 발견되거나 빈사 상태로 인해 안락사된 마카크는 말기 희생된 마카크와 동일한 방식으로 평가된다. 전체 조직 세트가 수집되고 임의의 총체적인 병변이 기록될 것이다.
추가적으로, 모든 마카크는 마취될 때마다 육안으로 검사된다. 부검시에, 마카크는 총체적인 이상이 있는지 검사한다. 모든 변경사항이 기록된다. 마카크는 연구 시작시, 부검시, 그리고 이들이 진정되는 모든 시점에 칭량한다.
식품 소비는 모니터링되지 않는다. 물은 임의로 투여되고, 농축 식품이 포함된 표준 식단이 마카크에게 제공된다.
모니터링을 위해 선택된 날에, 감각 신경 전도 연구가 수행된다.
신경학적 검사의 경우, 모니터링을 위해 선택된 날에, 비인간 영장류 신경학적 평가가 수행된다. 신경학적 평가는 5개 섹션으로 나뉜다: 지적 활동(Mentation), 자세 및 보행, 고유 감각, 뇌신경 및 척추 반사.
사후 분석을 위해, 빈사 상태에서 안락사되거나 죽은 채로 발견된 마카크를 비롯하여, 모든 마카크에 대해 총체적인 사후 검사가 수행된다. 모든 비정상적인 관찰이 기록된다.
본 연구는 동물에 대한 지속적인 평가를 필요로 하기 때문에, 부검 시간은 추후 시점에서 결정된다. 예기치 않게 죽은 임의의 동물은 가능한 한 빨리 부검한다. 모든 예정되지 않은 사망의 경우, 연구 병리학자의 재량에 따라 수집된 전체 조직 목록에 대해 임상 병리학, 광범위한 총체적인 병리학, 및 조직병리학이 수행된다. 가능한 사망 원인을 결정하기 위한 시도에 적절한 것으로 다른 분석 (면역 반응 등)이 포함된다. 조직은 표 6에 요약된 바와 같이 모든 동물에서 수집된다. 조직병리학이 적절하지 않은 부검시 이루어진 총체적 관찰(예를 들어, 체액, 헝클어진 모발, 결실된 해부학적 부분)은 수집되지 않는다.
연구 기간의 종료까지 생존한 마카크는 안락사된다. 마카크는 먼저 진정되고, 그 다음 안락사시킨다. 심장 박동 및 호흡의 부재로 사망이 확인된다. 마카크는 사망을 보장하기 위해 방혈될 수 있다.
표 6에 열거된 모든 조직이 보존된다. 조직은 파라핀 포매를 위해 10% 중성 완충 포르말린에 배치하여 고정된다. 조직병리학적 검사에 사용되는 안구는 파라핀 포매 전에 변형된 데이비슨 용액에 고정된다.
생체내 분포 분석을 위해, 표 6의 각 조직 절편은 가능한 한 빨리 -80℃로 동결된다. 연구 책임자의 재량에 따라, 조직으로부터 DNA를 추출하고 벡터 생체내 분포를 정량적 PCR로 평가한다.
조직병리학적 분석을 위해, 표 6의 하위 집합 또는 모든 조직을 헤마톡실린 및 에오신(H&E)으로 염색한다. 연구 병리학자의 재량에 따라 추가 절차 및/또는 다른 염색을 사용하여 조직학적 특징을 식별/명확하게 할 수 있으며, 이는 최종 보고서에 문서화된다. 실험 세부사항, 연구 절차 및 관찰을 문서화하는 모든 데이터는 연구 바인더에 기록되고 유지된다. 연구 완료시, 모든 보고서 및 원시 데이터는 아기록 보관소에 유지된다. 보존된 표본 및 조직은 보관되고 저장된다. 연구 책임자는 이러한 자료의 최종 배치에 대한 필요성을 결정한다. 실험 세부사항 및 연구 절차 및 관찰을 문서화하는 모든 데이터는 GTP 담당자에 의해 전용 노트북 및 연구 바인더에 기록되고 유지된다.
부검시 수집된 조직에 대해 수행되는 분석
연구의 결론에 따라, 마카크는 전체 병리학을 위해 수확된 조직으로 부검된다(부검시에 수집되는 조직 목록의 경우 표 6 참조).
조직병리학의 경우, 연구 책임자의 재량에 따라 조직병리학 수집을 위해 열거된 조직의 전체 또는 하위 집합에 대해 헤마톡실린 및 에오신(H&E) 염색을 수행한다. 추가적인 적절한 염색은 조직병리학적 소견에 기초하여 사용될 수 있다. Mfn2 cDNA 및 miRNA 발현의 경우, 포르말린 및 파라핀 포매(FFPE)에 보존된 조직 절편을 처리하고, 운동 뉴런을 레이저-캡처 미세절단한다. 척수로부터 분리된 운동 뉴런은 RNA 추출되고, qPCR은 특정 프라이머 세트를 사용하여 Mfn2 넉다운 수준, Mfn2 cDNA 발현 수준 및 miRNA 발현 수준을 결정하기 위해 수행된다. Mfn2의 넉다운 및 Mfn2 cDNA의 발현은 또한 qPCR 및 웨스턴 블롯에 의해 조직 샘플 용해물에서 평가될 수 있다. Mfn2에 대한 면역조직화학은 뇌 및 척수 조직에 대해 수행될 수 있다. 간략하게, 파라핀 절편은 Mfn2 단백질에 대해 생성된 항체와 함께 배양된다. 생체내 분포를 위해, 표 6의 각 조직 절편의 절편은 가능한 한 빨리 ≤ -60℃로 동결된다. DNA는 조직으로부터 추출될 수 있으며, 벡터 생체내 분포는 정량적 PCR에 의해 평가된다. 조직 림프구 분리 및 ELISPOT의 경우, 비장 및 골수로부터 림프구를 수확할 수 있으며, 캡시드 및 전이유전자 T 세포 반응을 위한 ELISPOT이 수행된다.
(서열목록 자유 텍스트)
숫자 식별자 <223> 하에서 자유 텍스트를 포함하는 서열에 대해 하기 정보가 제공된다.
본 명세서에 열거된 모든 특허, 특허 간행물, 및 기타 간행물, 뿐만 아니라 서열 목록 파일 "20-9141PCT_SeqListing_ST25"은 본원에 참조로 포함된다. 2020년 7월 13일자로 출원된 미국 특허 가출원 제63/051,336호 및 2021년 4월 9일자로 출원된 미국 특허 가출원 제63/173,045호는 본원에 참조로 포함된다. 본 발명은 특히 바람직한 구현예를 참조하여 기술되었지만, 본 발명의 사상을 벗어나지 않으면서 변형이 이루어질 수 있음이 인식될 것이다. 해당 변형은 첨부된 청구범위의 범주 내에 속하는 것으로 의도된다.
SEQUENCE LISTING
<110> The Trustees of The University of Pennsylvania
<120> COMPOSITIONS USEFUL FOR TREATMENT OF CHARCOT-MARIE-TOOTH DISEASE
<130> UPN-20-9141.PCT
<150> US 63/051,336
<151> 2020-07-13
<150> US 63/173,045
<151> 2021-04-09
<160> 90
<170> PatentIn version 3.5
<210> 1
<211> 4585
<212> DNA
<213> Artificial Sequence
<220>
<223> Vector Genome Syn.PI.hMfn2opt.link.hMfn2 miR1693.WPRE.bGH
<220>
<221> repeat_region
<222> (1)..(141)
<223> 5'ITR
<220>
<221> promoter
<222> (223)..(682)
<223> hSynapsin
<220>
<221> Intron
<222> (694)..(826)
<223> Promega Chimeric Intron
<220>
<221> misc_signal
<222> (857)..(862)
<223> Kozak
<220>
<221> CDS
<222> (863)..(3136)
<223> human Mfn2 engineered
<220>
<221> misc_feature
<222> (3134)..(3139)
<223> Dbl stop codon
<220>
<221> misc_feature
<222> (3140)..(3229)
<223> linker
<220>
<221> misc_binding
<222> (3230)..(3252)
<223> 5'flank
<220>
<221> misc_feature
<222> (3253)..(3316)
<223> hMfn2 miR1693
<220>
<221> misc_binding
<222> (3317)..(3360)
<223> 3'flank
<220>
<221> misc_feature
<222> (3463)..(4045)
<223> WRPE
<220>
<221> misc_feature
<222> (4410)..(4455)
<223> Additional AAV squences
<220>
<221> repeat_region
<222> (4456)..(4585)
<223> 3'ITR
<400> 1
ccttaattag gctgcgcgct cgctcgctca ctgaggccgg gcgaccaaag gtcgcccgac 60
gcccgggctt tgcccgggcg gcctcagtga gcgagcgagc gcgcagagag ggagtggcca 120
actccatcac taggggttcc ttgtagttaa tgattaaccc gccatgctac ttatctacgt 180
agccatgctc taggaagatc ggaattcgcc cttaagctag actcgagctg cagagggccc 240
tgcgtatgag tgcaagtggg ttttaggacc aggatgaggc ggggtggggg tgcctacctg 300
acgaccgacc ccgacccact ggacaagcac ccaaccccca ttccccaaat tgcgcatccc 360
ctatcagaga gggggagggg aaacaggatg cggcgaggcg cgtgcgcact gccagcttca 420
gcaccgcgga cagtgccttc gcccccgcct ggcggcgcgc gccaccgccg cctcagcact 480
gaaggcgcgc tgacgtcact cgccggtccc ccgcaaactc cccttcccgg ccaccttggt 540
cgcgtccgcg ccgccgccgg cccagccgga ccgcaccacg cgaggcgcga gatagggggg 600
cacgggcgcg accatctgcg ctgcggcgcc ggcgactcag cgctgcctca gtctgcggtg 660
ggcagcggag gagtcgtgtc gtgcctgaga gcggtaagta tcaaggttac aagacaggtt 720
taaggagacc aatagaaact gggcttgtcg agacagagaa gactcttgcg tttctgatag 780
gcacctattg gtcttactga catccacttt gcctttctct ccacagtacg tagaattcac 840
gcgtgctagc accggtgcca cc atg agc ctg ctg ttc agc cgg tgc aac agc 892
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser
1 5 10
atc gtg acc gtg aag aaa aac aag cgg cac atg gcc gaa gtg aac gcc 940
Ile Val Thr Val Lys Lys Asn Lys Arg His Met Ala Glu Val Asn Ala
15 20 25
tct cca ctg aag cac ttc gtg acc gcc aag aag aag atc aac ggc atc 988
Ser Pro Leu Lys His Phe Val Thr Ala Lys Lys Lys Ile Asn Gly Ile
30 35 40
ttc gag cag ctg ggc gcc tac atc caa gag agc gcc acc ttc ctg gaa 1036
Phe Glu Gln Leu Gly Ala Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu
45 50 55
gat acc tac aga aac gcc gag ctg gac ccc gtg acc aca gag gaa cag 1084
Asp Thr Tyr Arg Asn Ala Glu Leu Asp Pro Val Thr Thr Glu Glu Gln
60 65 70
gtg ctg gat gtg aag ggc tac ctg agc aaa gtg cgg ggc atc tct gaa 1132
Val Leu Asp Val Lys Gly Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu
75 80 85 90
gtg ctg gcc aga cgg cat atg aag gtg gcc ttt ttc ggc cgg acc agc 1180
Val Leu Ala Arg Arg His Met Lys Val Ala Phe Phe Gly Arg Thr Ser
95 100 105
aac ggc aag agc acc gtg atc aat gcc atg ctg tgg gac aaa gtg ctg 1228
Asn Gly Lys Ser Thr Val Ile Asn Ala Met Leu Trp Asp Lys Val Leu
110 115 120
ccc tct gga atc ggc cac acc acc aac tgc ttt ctg aga gtg gaa ggc 1276
Pro Ser Gly Ile Gly His Thr Thr Asn Cys Phe Leu Arg Val Glu Gly
125 130 135
acc gac ggc cac gag gca ttt ctg ctg aca gag ggc tcc gag gaa aag 1324
Thr Asp Gly His Glu Ala Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys
140 145 150
cgg agc gcc aag aca gtg aac cag ctg gcc cat gct ctg cac cag gat 1372
Arg Ser Ala Lys Thr Val Asn Gln Leu Ala His Ala Leu His Gln Asp
155 160 165 170
aag cag ctg cat gcc gga agc ctg gtg tcc gtg atg tgg ccc aat agc 1420
Lys Gln Leu His Ala Gly Ser Leu Val Ser Val Met Trp Pro Asn Ser
175 180 185
aag tgc cct ctg ctg aag gac gac ctg gtg ctg atg gat agc ccc ggg 1468
Lys Cys Pro Leu Leu Lys Asp Asp Leu Val Leu Met Asp Ser Pro Gly
190 195 200
atc gat gtg acc acc gaa ctg gac agc tgg atc gac aag ttc tgc ctg 1516
Ile Asp Val Thr Thr Glu Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu
205 210 215
gac gcc gac gtg ttc gtg ctg gtg gcc aat agc gag agc acc ctg atg 1564
Asp Ala Asp Val Phe Val Leu Val Ala Asn Ser Glu Ser Thr Leu Met
220 225 230
cag acc gag aag cac ttt ttc cac aag gtg tcc gag cgg ctg agc aga 1612
Gln Thr Glu Lys His Phe Phe His Lys Val Ser Glu Arg Leu Ser Arg
235 240 245 250
ccc aat atc ttt atc ctg aac aac aga tgg gac gcc agc gcc agc gag 1660
Pro Asn Ile Phe Ile Leu Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu
255 260 265
ccc gag tat atg gaa gaa gtg cgg cgg cag cat atg gaa cgg tgc aca 1708
Pro Glu Tyr Met Glu Glu Val Arg Arg Gln His Met Glu Arg Cys Thr
270 275 280
tcc ttt ctg gtg gac gag ctg ggc gtc gtg gat aga tct cag gcc ggc 1756
Ser Phe Leu Val Asp Glu Leu Gly Val Val Asp Arg Ser Gln Ala Gly
285 290 295
gac aga atc ttc ttt gtg tcc gcc aaa gag gtg ctg aac gcc cgg att 1804
Asp Arg Ile Phe Phe Val Ser Ala Lys Glu Val Leu Asn Ala Arg Ile
300 305 310
cag aaa gcc cag gga atg cct gaa ggc gga ggt gca ctg gcc gag gga 1852
Gln Lys Ala Gln Gly Met Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly
315 320 325 330
ttt caa gtg cgg atg ttc gag ttc cag aac ttc gag cgg aga ttc gag 1900
Phe Gln Val Arg Met Phe Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu
335 340 345
gag tgc atc agc cag agc gcc gtc aag acc aag ttc gag cag cat acc 1948
Glu Cys Ile Ser Gln Ser Ala Val Lys Thr Lys Phe Glu Gln His Thr
350 355 360
gtg cgg gcc aag cag att gcc gaa gcc gtc aga ctg atc atg gac agc 1996
Val Arg Ala Lys Gln Ile Ala Glu Ala Val Arg Leu Ile Met Asp Ser
365 370 375
ctg cat atg gcc gcc aga gag cag cag gtc tac tgc gag gaa atg cgg 2044
Leu His Met Ala Ala Arg Glu Gln Gln Val Tyr Cys Glu Glu Met Arg
380 385 390
gaa gag aga cag gac cgg ctg aag ttc atc gac aag cag ctg gaa ctg 2092
Glu Glu Arg Gln Asp Arg Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu
395 400 405 410
ctg gcc cag gac tac aag ctg cgg atc aag cag atc acc gaa gag gtg 2140
Leu Ala Gln Asp Tyr Lys Leu Arg Ile Lys Gln Ile Thr Glu Glu Val
415 420 425
gaa aga cag gtg tcc acc gct atg gcc gag gaa atc aga cgg ctg agc 2188
Glu Arg Gln Val Ser Thr Ala Met Ala Glu Glu Ile Arg Arg Leu Ser
430 435 440
gtg ctg gtc gac gac tac cag atg gac ttt cac ccc tct cca gtg gtg 2236
Val Leu Val Asp Asp Tyr Gln Met Asp Phe His Pro Ser Pro Val Val
445 450 455
ctg aaa gtc tac aaa aac gag ctg cac cgg cac atc gag gaa ggc ctg 2284
Leu Lys Val Tyr Lys Asn Glu Leu His Arg His Ile Glu Glu Gly Leu
460 465 470
ggc aga aac atg agc gac aga tgc agc acc gcc atc acc aat agc ctg 2332
Gly Arg Asn Met Ser Asp Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu
475 480 485 490
cag acc atg cag cag gac atg atc gac ggc ctg aaa cct ctg ctg cct 2380
Gln Thr Met Gln Gln Asp Met Ile Asp Gly Leu Lys Pro Leu Leu Pro
495 500 505
gtg tcc gtc aga tcc cag atc gat atg ctg gtg ccc cgg cag tgc ttt 2428
Val Ser Val Arg Ser Gln Ile Asp Met Leu Val Pro Arg Gln Cys Phe
510 515 520
agc ctg aac tac gac ctg aac tgc gac aag ctg tgc gcc gat ttc caa 2476
Ser Leu Asn Tyr Asp Leu Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln
525 530 535
gag gac atc gag ttt cac ttc agc ctc ggc tgg aca atg ctg gtc aac 2524
Glu Asp Ile Glu Phe His Phe Ser Leu Gly Trp Thr Met Leu Val Asn
540 545 550
aga ttt ctg ggc ccc aag aac agc aga cgg gcc ctg atg ggc tac aac 2572
Arg Phe Leu Gly Pro Lys Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn
555 560 565 570
gat cag gtg cag agg ccc att cct ctg aca ccc gcc aat cct agc atg 2620
Asp Gln Val Gln Arg Pro Ile Pro Leu Thr Pro Ala Asn Pro Ser Met
575 580 585
cct cca ctg cct cag ggc agc ctg aca caa gag gaa ttc atg gtg tct 2668
Pro Pro Leu Pro Gln Gly Ser Leu Thr Gln Glu Glu Phe Met Val Ser
590 595 600
atg gtc acc ggc ctg gcc agc ctg acc agc aga aca tct atg ggc atc 2716
Met Val Thr Gly Leu Ala Ser Leu Thr Ser Arg Thr Ser Met Gly Ile
605 610 615
ctg gtc gtc ggc ggc gtt gtg tgg aaa gct gtt ggc tgg cgg ctg atc 2764
Leu Val Val Gly Gly Val Val Trp Lys Ala Val Gly Trp Arg Leu Ile
620 625 630
gcc ctg agc ttt ggc ctg tat ggc ctg ctg tac gtg tac gag aga ctg 2812
Ala Leu Ser Phe Gly Leu Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu
635 640 645 650
acc tgg acc acc aag gcc aaa gag cgg gcc ttc aag cgg cag ttt gtg 2860
Thr Trp Thr Thr Lys Ala Lys Glu Arg Ala Phe Lys Arg Gln Phe Val
655 660 665
gaa cac gcc tcc gag aaa ctg cag ctg gtg atc agc tac acc ggc agc 2908
Glu His Ala Ser Glu Lys Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser
670 675 680
aat tgc agc cac cag gtg cag caa gag ctg tcc gga aca ttc gcc cac 2956
Asn Cys Ser His Gln Val Gln Gln Glu Leu Ser Gly Thr Phe Ala His
685 690 695
ctg tgt cag cag gtc gac gtg acc aga gag aac ctg gaa caa gag atc 3004
Leu Cys Gln Gln Val Asp Val Thr Arg Glu Asn Leu Glu Gln Glu Ile
700 705 710
gcc gcc atg aat aag aaa atc gag gtg ctc gac tcc ctg cag agc aag 3052
Ala Ala Met Asn Lys Lys Ile Glu Val Leu Asp Ser Leu Gln Ser Lys
715 720 725 730
gcc aag ctg ctg aga aac aag gcc ggc tgg ctg gac agc gag ctg aat 3100
Ala Lys Leu Leu Arg Asn Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn
735 740 745
atg ttc acc cac cag tac ctg cag cct agc cgc taa taatgtacaa 3146
Met Phe Thr His Gln Tyr Leu Gln Pro Ser Arg
750 755
gtaaagcgcc cgcaggcttg cacccgtacc tttgggagcg cgcgccctcg tcgtgtcgtg 3206
acgtcacccg ttctgttgga tccctggagg cttgctgaag gctgtatgct gttcttataa 3266
accttgagga ctgttttggc cactgactga cagtcctcag tttataagaa caggacacaa 3326
ggcctgttac tagcactcac atggaacaaa tggcccagat ctagggtggg gccacctgcc 3386
ggtaggtgtg cggtaggctt ttctccgtcg caggacgcag ggttcgggcc tagcttaagc 3446
ttctcgagat cgataatcaa cctctggatt acaaaatttg tgaaagattg actggtattc 3506
ttaactatgt tgctcctttt acgctatgtg gatacgctgc tttaatgcct ttgtatcatg 3566
ctattgcttc ccgtatggct ttcattttct cctccttgta taaatcctgg ttgctgtctc 3626
tttatgagga gttgtggccc gttgtcaggc aacgtggcgt ggtgtgcact gtgtttgctg 3686
acgcaacccc cactggttgg ggcattgcca ccacctgtca gctcctttcc gggactttcg 3746
ctttccccct ccctattgcc acggcggaac tcatcgccgc ctgccttgcc cgctgctgga 3806
caggggctcg gctgttgggc actgacaatt ccgtggtgtt gtcggggaaa tcatcgtcct 3866
ttccttggct gctcgcctgt gttgccacct ggattctgcg cgggacgccc ttctgctacg 3926
tcccttcggc cctcaatcca gcggaccttc cttcccgcgg cctgctgccg gctctgcggc 3986
ctcttccgcg tcttcgcctt cgccctcaga cgagtcggat ctccctttgg gccgcctccc 4046
cgcctgctga tcgccctgag cctggccctg gtgaccaaca gccaggtgca attgctagag 4106
tcgactctag agcggccgcc taaggctcga ctagagctcg ctgatcagcc tcgactgtgc 4166
cttctagttg ccagccatct gttgtttgcc cctcccccgt gccttccttg accctggaag 4226
gtgccactcc cactgtcctt tcctaataaa atgaggaaat tgcatcgcat tgtctgagta 4286
ggtgtcattc tattctgggg ggtggggtgg ggcaggacag caagggggag gattgggaag 4346
acaatagcag gcatgctggg gactcgagtt aagggcgaat tcccgataag gatcttccta 4406
gagcatggct acgtagataa gtagcatggc gggttaatca ttaactacaa ggaaccccta 4466
gtgatggagt tggccactcc ctctctgcgc gctcgctcgc tcactgaggc cgggcgacca 4526
aaggtcgccc gacgcccggg ctttgcccgg gcggcctcag tgagcgagcg agcgcgcag 4585
<210> 2
<211> 757
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 2
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
Asn Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala
50 55 60
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
Thr Thr Asn Cys Phe Leu Arg Val Glu Gly Thr Asp Gly His Glu Ala
130 135 140
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Arg Ser Ala Lys Thr Val
145 150 155 160
Asn Gln Leu Ala His Ala Leu His Gln Asp Lys Gln Leu His Ala Gly
165 170 175
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys His Phe
225 230 235 240
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
Leu Gly Val Val Asp Arg Ser Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
Ser Ala Lys Glu Val Leu Asn Ala Arg Ile Gln Lys Ala Gln Gly Met
305 310 315 320
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Met Ala Ala Arg
370 375 380
Glu Gln Gln Val Tyr Cys Glu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
Leu Arg Ile Lys Gln Ile Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Asp Tyr
435 440 445
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Ser Gln
500 505 510
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu
515 520 525
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
Ile Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
Ser Leu Thr Gln Glu Glu Phe Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala
645 650 655
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu His Ala Ser Glu Lys
660 665 670
Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
Val Thr Arg Glu Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
Ile Glu Val Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Thr His Gln Tyr
740 745 750
Leu Gln Pro Ser Arg
755
<210> 3
<211> 4560
<212> DNA
<213> Artificial Sequence
<220>
<223> Vector Genome Syn.PI.rMnf2opt.link.rMfn2 miR1518 WPRE.BGH
<220>
<221> repeat_region
<222> (1)..(141)
<223> 5'ITR
<220>
<221> promoter
<222> (223)..(682)
<223> hSynapsin
<220>
<221> Intron
<222> (694)..(826)
<223> Promega Chimeric Intron
<220>
<221> CDS
<222> (863)..(3133)
<223> rMfn2 engineered
<220>
<221> misc_feature
<222> (3134)..(3139)
<223> Dbl stop codon
<220>
<221> misc_feature
<222> (3140)..(3229)
<223> linker
<220>
<221> misc_signal
<222> (3230)..(3252)
<223> 5'flank
<220>
<221> misc_feature
<222> (3253)..(3316)
<223> rMfn2 miR1518
<220>
<221> misc_signal
<222> (3317)..(3360)
<223> 3'flank
<220>
<221> enhancer
<222> (3457)..(4044)
<223> WRPE
<220>
<221> misc_feature
<222> (4385)..(4430)
<223> Additional AAV sequences
<220>
<221> repeat_region
<222> (4431)..(4560)
<223> 3'ITR
<400> 3
ccttaattag gctgcgcgct cgctcgctca ctgaggccgg gcgaccaaag gtcgcccgac 60
gcccgggctt tgcccgggcg gcctcagtga gcgagcgagc gcgcagagag ggagtggcca 120
actccatcac taggggttcc ttgtagttaa tgattaaccc gccatgctac ttatctacgt 180
agccatgctc taggaagatc ggaattcgcc cttaagctag actcgagctg cagagggccc 240
tgcgtatgag tgcaagtggg ttttaggacc aggatgaggc ggggtggggg tgcctacctg 300
acgaccgacc ccgacccact ggacaagcac ccaaccccca ttccccaaat tgcgcatccc 360
ctatcagaga gggggagggg aaacaggatg cggcgaggcg cgtgcgcact gccagcttca 420
gcaccgcgga cagtgccttc gcccccgcct ggcggcgcgc gccaccgccg cctcagcact 480
gaaggcgcgc tgacgtcact cgccggtccc ccgcaaactc cccttcccgg ccaccttggt 540
cgcgtccgcg ccgccgccgg cccagccgga ccgcaccacg cgaggcgcga gatagggggg 600
cacgggcgcg accatctgcg ctgcggcgcc ggcgactcag cgctgcctca gtctgcggtg 660
ggcagcggag gagtcgtgtc gtgcctgaga gcggtaagta tcaaggttac aagacaggtt 720
taaggagacc aatagaaact gggcttgtcg agacagagaa gactcttgcg tttctgatag 780
gcacctattg gtcttactga catccacttt gcctttctct ccacagtacg tagaattcac 840
gcgtgctagc accggtgcca cc atg tct ctg ctg ttc agc cgg tgc aac agc 892
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser
1 5 10
atc gtg acc gtg aag aaa gac aag agg cac atg gcc gaa gtg aac gcc 940
Ile Val Thr Val Lys Lys Asp Lys Arg His Met Ala Glu Val Asn Ala
15 20 25
tct cca ctg aag cac ttc gtg acc gcc aag aag aag atc aac ggc atc 988
Ser Pro Leu Lys His Phe Val Thr Ala Lys Lys Lys Ile Asn Gly Ile
30 35 40
ttc gag cag ctg ggc gcc tac atc caa gag tct gcc ggc ttc ctg gaa 1036
Phe Glu Gln Leu Gly Ala Tyr Ile Gln Glu Ser Ala Gly Phe Leu Glu
45 50 55
gat acc cac aga aac acc gag ctg gac ccc gtg acc aca gag gaa cag 1084
Asp Thr His Arg Asn Thr Glu Leu Asp Pro Val Thr Thr Glu Glu Gln
60 65 70
gtg ctg gac gtg aag ggc tac ctg tct aaa gtg cgg ggc atc agc gag 1132
Val Leu Asp Val Lys Gly Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu
75 80 85 90
gtg ctg gct aga agg cat atg aag gtg gcc ttt ttc ggc agg acc agc 1180
Val Leu Ala Arg Arg His Met Lys Val Ala Phe Phe Gly Arg Thr Ser
95 100 105
aac ggc aag agc acc gtg atc aac gcc atg ctg tgg gac aaa gtg ctg 1228
Asn Gly Lys Ser Thr Val Ile Asn Ala Met Leu Trp Asp Lys Val Leu
110 115 120
cct tct ggc atc ggc cac acc acc aac tgc ttt ctg aga gtc ggc ggc 1276
Pro Ser Gly Ile Gly His Thr Thr Asn Cys Phe Leu Arg Val Gly Gly
125 130 135
aca gac ggc cac gag gct ttt ttg ctg acc gag ggc tcc gaa gag aag 1324
Thr Asp Gly His Glu Ala Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys
140 145 150
aaa tcc gtg aaa acc gtg aac cag ctg gcc cac gct ctg cac cag gat 1372
Lys Ser Val Lys Thr Val Asn Gln Leu Ala His Ala Leu His Gln Asp
155 160 165 170
gaa caa ctg cac gcc gga agc ctg gtg tcc gtg atg tgg cct aac agc 1420
Glu Gln Leu His Ala Gly Ser Leu Val Ser Val Met Trp Pro Asn Ser
175 180 185
aag tgc cct ctg ctg aag gac gac ctg gtg ctg atg gac tct cct gga 1468
Lys Cys Pro Leu Leu Lys Asp Asp Leu Val Leu Met Asp Ser Pro Gly
190 195 200
atc gac gtg acc act gag ctg gac agc tgg atc gac aag ttc tgc ctg 1516
Ile Asp Val Thr Thr Glu Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu
205 210 215
gac gcc gac gtg ttc gtg ctg gtg gct aac tct gag agc acc ctg atg 1564
Asp Ala Asp Val Phe Val Leu Val Ala Asn Ser Glu Ser Thr Leu Met
220 225 230
cag acc gag aag cag ttc ttc cac aag gtg tcc gag agg ctg agc agg 1612
Gln Thr Glu Lys Gln Phe Phe His Lys Val Ser Glu Arg Leu Ser Arg
235 240 245 250
ccc aat atc ttt atc ctg aac aac aga tgg gac gcc agc gcc agc gag 1660
Pro Asn Ile Phe Ile Leu Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu
255 260 265
ccc gag tat atg gaa gaa gtg cgg agg cag cat atg gaa agg tgt acc 1708
Pro Glu Tyr Met Glu Glu Val Arg Arg Gln His Met Glu Arg Cys Thr
270 275 280
agc ttc ctg gtg gac gag ctg gga gtc gtg gat aga gca cag gcc ggc 1756
Ser Phe Leu Val Asp Glu Leu Gly Val Val Asp Arg Ala Gln Ala Gly
285 290 295
gac aga atc ttc ttc gtg tct gcc aaa gag gtg ctg agc gcc agg gtg 1804
Asp Arg Ile Phe Phe Val Ser Ala Lys Glu Val Leu Ser Ala Arg Val
300 305 310
cag aaa gcc cag gga atg cct gaa ggc ggc gga gct ttg gcc gag gga 1852
Gln Lys Ala Gln Gly Met Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly
315 320 325 330
ttt caa gtg cgg atg ttc gag ttc cag aac ttc gag cgg aga ttc gag 1900
Phe Gln Val Arg Met Phe Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu
335 340 345
gaa tgc atc agc cag agc gcc gtc aag aca aag ttc gag cag cac aca 1948
Glu Cys Ile Ser Gln Ser Ala Val Lys Thr Lys Phe Glu Gln His Thr
350 355 360
gtg cgg gcc aag cag atc gct gag gct gtg cgg ctg atc atg gac agc 1996
Val Arg Ala Lys Gln Ile Ala Glu Ala Val Arg Leu Ile Met Asp Ser
365 370 375
ctg cat atc gcc gct caa gag cag agg gtg tac tgc ctg gaa atg cgg 2044
Leu His Ile Ala Ala Gln Glu Gln Arg Val Tyr Cys Leu Glu Met Arg
380 385 390
gaa gag agg cag gac agg ctg aga ttc atc gac aag cag ctg gaa ctg 2092
Glu Glu Arg Gln Asp Arg Leu Arg Phe Ile Asp Lys Gln Leu Glu Leu
395 400 405 410
ctg gcc cag gac tac aag ctg agg atc aag cag atg acc gaa gag gtg 2140
Leu Ala Gln Asp Tyr Lys Leu Arg Ile Lys Gln Met Thr Glu Glu Val
415 420 425
gaa aga cag gtg tcc acc gcc atg gcc gag gaa atc cgt aga ctg tct 2188
Glu Arg Gln Val Ser Thr Ala Met Ala Glu Glu Ile Arg Arg Leu Ser
430 435 440
gtg ctg gtc gac gag tac cag atg gac ttt cac ccc tct cca gtg gtg 2236
Val Leu Val Asp Glu Tyr Gln Met Asp Phe His Pro Ser Pro Val Val
445 450 455
ctg aag gtc tac aaa aac gag ctg cac agg cac atc gag gaa ggc ctg 2284
Leu Lys Val Tyr Lys Asn Glu Leu His Arg His Ile Glu Glu Gly Leu
460 465 470
ggc aga aac atg agc gac agg tgc tct acc gct atc gcc agc agc ctg 2332
Gly Arg Asn Met Ser Asp Arg Cys Ser Thr Ala Ile Ala Ser Ser Leu
475 480 485 490
cag aca atg cag cag gac atg atc gac ggc ctg aag cct ctg ctg cct 2380
Gln Thr Met Gln Gln Asp Met Ile Asp Gly Leu Lys Pro Leu Leu Pro
495 500 505
gtg tct gtg cgg aac cag atc gat atg ctg gtg ccc agg cag tgc ttc 2428
Val Ser Val Arg Asn Gln Ile Asp Met Leu Val Pro Arg Gln Cys Phe
510 515 520
tcc ctg tcc tac gac ctg aac tgc gac aag ctg tgt gcc gac ttc caa 2476
Ser Leu Ser Tyr Asp Leu Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln
525 530 535
gag gac atc gag ttt cac ttc agc ctc ggc tgg aca atg ctg gtc aac 2524
Glu Asp Ile Glu Phe His Phe Ser Leu Gly Trp Thr Met Leu Val Asn
540 545 550
aga ttc ctg gga cct aag aac tcc aga cgg gcc ctg ctg gga tac aac 2572
Arg Phe Leu Gly Pro Lys Asn Ser Arg Arg Ala Leu Leu Gly Tyr Asn
555 560 565 570
gat cag gtg caa agg ccc ctg cct ctg aca cca gct aac cct tct atg 2620
Asp Gln Val Gln Arg Pro Leu Pro Leu Thr Pro Ala Asn Pro Ser Met
575 580 585
cct cct ctg cct caa ggc tct ctg acc caa gag gaa ctg atg gtg tcc 2668
Pro Pro Leu Pro Gln Gly Ser Leu Thr Gln Glu Glu Leu Met Val Ser
590 595 600
atg gtc aca ggc ctg gct tcc ctg acc agc aga acc tct atg ggc atc 2716
Met Val Thr Gly Leu Ala Ser Leu Thr Ser Arg Thr Ser Met Gly Ile
605 610 615
ctg gtc gtc ggc gga gtt gtg tgg aaa gct gtt ggc tgg cgc ctg atc 2764
Leu Val Val Gly Gly Val Val Trp Lys Ala Val Gly Trp Arg Leu Ile
620 625 630
gcc ctg agc ttt gga ctg tac gga ctg ctg tac gtg tac gag aga ctg 2812
Ala Leu Ser Phe Gly Leu Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu
635 640 645 650
acc tgg acc acc agg gcc aaa gag agg gcc ttc aag agg cag ttc gtg 2860
Thr Trp Thr Thr Arg Ala Lys Glu Arg Ala Phe Lys Arg Gln Phe Val
655 660 665
gaa tac gcc tcc gag aaa ctg cag ctg att atc tcc tac acc ggc agc 2908
Glu Tyr Ala Ser Glu Lys Leu Gln Leu Ile Ile Ser Tyr Thr Gly Ser
670 675 680
aac tgc agc cac cag gtg cag caa gag ctg tct gga aca ttc gcc cac 2956
Asn Cys Ser His Gln Val Gln Gln Glu Leu Ser Gly Thr Phe Ala His
685 690 695
ctg tgc cag cag gtc gac atc acc aga gac aac ctg gaa caa gag atc 3004
Leu Cys Gln Gln Val Asp Ile Thr Arg Asp Asn Leu Glu Gln Glu Ile
700 705 710
gcc gct atg aat aag aag gtg gaa gcc ctg gac tcc ctg cag agc aag 3052
Ala Ala Met Asn Lys Lys Val Glu Ala Leu Asp Ser Leu Gln Ser Lys
715 720 725 730
gct aag ctg ctg aga aac aag gcc ggc tgg ctg gac tcc gag ctg aat 3100
Ala Lys Leu Leu Arg Asn Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn
735 740 745
atg ttt atc cac cag tac ctg cag cct agc cgc tgatgatgta caagtaaagc 3153
Met Phe Ile His Gln Tyr Leu Gln Pro Ser Arg
750 755
ggccgcaagc ttgcacccgt acctttggga gcgcgcgccc tcgtcgtgtc gtgacgtcac 3213
ccgttctgtt ggatccctgg aggcttgctg aaggctgtat gctgttctta taaaccttga 3273
ggacagtttt ggccactgac tgactgtcct cagtttataa gaacaggaca caaggcctgt 3333
tactagcact cacatggaac aaatggccca gatctagggt ggggccacct gccggtaggt 3393
gtgcggtagg cttttctccg tcgcaggacg cagggttcgg gcctagcttc tcgagatcga 3453
taatcaacct ctggattaca aaatttgtga aagattgact ggtattctta actatgttgc 3513
tccttttacg ctatgtggat acgctgcttt aatgcctttg tatcatgcta ttgcttcccg 3573
tatggctttc attttctcct ccttgtataa atcctggttg ctgtctcttt atgaggagtt 3633
gtggcccgtt gtcaggcaac gtggcgtggt gtgcactgtg tttgctgacg caacccccac 3693
tggttggggc attgccacca cctgtcagct cctttccggg actttcgctt tccccctccc 3753
tattgccacg gcggaactca tcgccgcctg ccttgcccgc tgctggacag gggctcggct 3813
gttgggcact gacaattccg tggtgttgtc ggggaaatca tcgtcctttc cttggctgct 3873
cgcctgtgtt gccacctgga ttctgcgcgg gacgcccttc tgctacgtcc cttcggccct 3933
caatccagcg gaccttcctt cccgcggcct gctgccggct ctgcggcctc ttccgcgtct 3993
tcgccttcgc cctcagacga gtcggatctc cctttgggcc gcctccccgc ctgctgatcg 4053
ccctgagcct ggccctggtg accaacagcc aggtgcaatt gaagctttct agagtcgact 4113
agagctcgct gatcagcctc gactgtgcct tctagttgcc agccatctgt tgtttgcccc 4173
tcccccgtgc cttccttgac cctggaaggt gccactccca ctgtcctttc ctaataaaat 4233
gaggaaattg catcgcattg tctgagtagg tgtcattcta ttctgggggg tggggtgggg 4293
caggacagca agggggagga ttgggaagac aatagcaggc atgctgggga ctcgagttaa 4353
gggcgaattc ccgataagga tcttcctaga gcatggctac gtagataagt agcatggcgg 4413
gttaatcatt aactacaagg aacccctagt gatggagttg gccactccct ctctgcgcgc 4473
tcgctcgctc actgaggccg ggcgaccaaa ggtcgcccga cgcccgggct ttgcccgggc 4533
ggcctcagtg agcgagcgag cgcgcag 4560
<210> 4
<211> 757
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 4
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
Asp Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
Tyr Ile Gln Glu Ser Ala Gly Phe Leu Glu Asp Thr His Arg Asn Thr
50 55 60
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
Thr Thr Asn Cys Phe Leu Arg Val Gly Gly Thr Asp Gly His Glu Ala
130 135 140
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Lys Ser Val Lys Thr Val
145 150 155 160
Asn Gln Leu Ala His Ala Leu His Gln Asp Glu Gln Leu His Ala Gly
165 170 175
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys Gln Phe
225 230 235 240
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
Leu Gly Val Val Asp Arg Ala Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
Ser Ala Lys Glu Val Leu Ser Ala Arg Val Gln Lys Ala Gln Gly Met
305 310 315 320
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Ile Ala Ala Gln
370 375 380
Glu Gln Arg Val Tyr Cys Leu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
Leu Arg Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
Leu Arg Ile Lys Gln Met Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Glu Tyr
435 440 445
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
Arg Cys Ser Thr Ala Ile Ala Ser Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Asn Gln
500 505 510
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Ser Tyr Asp Leu
515 520 525
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
Asn Ser Arg Arg Ala Leu Leu Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
Leu Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
Ser Leu Thr Gln Glu Glu Leu Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Arg Ala
645 650 655
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu Tyr Ala Ser Glu Lys
660 665 670
Leu Gln Leu Ile Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
Ile Thr Arg Asp Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
Val Glu Ala Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Ile His Gln Tyr
740 745 750
Leu Gln Pro Ser Arg
755
<210> 5
<211> 141
<212> DNA
<213> Artificial Sequence
<220>
<223> 5' ITR
<400> 5
ccttaattag gctgcgcgct cgctcgctca ctgaggccgg gcgaccaaag gtcgcccgac 60
gcccgggctt tgcccgggcg gcctcagtga gcgagcgagc gcgcagagag ggagtggcca 120
actccatcac taggggttcc t 141
<210> 6
<211> 460
<212> DNA
<213> Artificial Sequence
<220>
<223> hSynapsin promoter
<400> 6
tcgagctgca gagggccctg cgtatgagtg caagtgggtt ttaggaccag gatgaggcgg 60
ggtgggggtg cctacctgac gaccgacccc gacccactgg acaagcaccc aacccccatt 120
ccccaaattg cgcatcccct atcagagagg gggaggggaa acaggatgcg gcgaggcgcg 180
tgcgcactgc cagcttcagc accgcggaca gtgccttcgc ccccgcctgg cggcgcgcgc 240
caccgccgcc tcagcactga aggcgcgctg acgtcactcg ccggtccccc gcaaactccc 300
cttcccggcc accttggtcg cgtccgcgcc gccgccggcc cagccggacc gcaccacgcg 360
aggcgcgaga taggggggca cgggcgcgac catctgcgct gcggcgccgg cgactcagcg 420
ctgcctcagt ctgcggtggg cagcggagga gtcgtgtcgt 460
<210> 7
<211> 133
<212> DNA
<213> Artificial Sequence
<220>
<223> Promega Chimeric Intron
<400> 7
gtaagtatca aggttacaag acaggtttaa ggagaccaat agaaactggg cttgtcgaga 60
cagagaagac tcttgcgttt ctgataggca cctattggtc ttactgacat ccactttgcc 120
tttctctcca cag 133
<210> 8
<211> 583
<212> DNA
<213> Artificial Sequence
<220>
<223> WPRE
<400> 8
tcaacctctg gattacaaaa tttgtgaaag attgactggt attcttaact atgttgctcc 60
ttttacgcta tgtggatacg ctgctttaat gcctttgtat catgctattg cttcccgtat 120
ggctttcatt ttctcctcct tgtataaatc ctggttgctg tctctttatg aggagttgtg 180
gcccgttgtc aggcaacgtg gcgtggtgtg cactgtgttt gctgacgcaa cccccactgg 240
ttggggcatt gccaccacct gtcagctcct ttccgggact ttcgctttcc ccctccctat 300
tgccacggcg gaactcatcg ccgcctgcct tgcccgctgc tggacagggg ctcggctgtt 360
gggcactgac aattccgtgg tgttgtcggg gaaatcatcg tcctttcctt ggctgctcgc 420
ctgtgttgcc acctggattc tgcgcgggac gcccttctgc tacgtccctt cggccctcaa 480
tccagcggac cttccttccc gcggcctgct gccggctctg cggcctcttc cgcgtcttcg 540
ccttcgccct cagacgagtc ggatctccct ttgggccgcc tcc 583
<210> 9
<211> 46
<212> DNA
<213> Artificial Sequence
<220>
<223> additonal AAV sequences
<400> 9
catggctacg tagataagta gcatggcggg ttaatcatta actaca 46
<210> 10
<211> 130
<212> DNA
<213> Artificial Sequence
<220>
<223> 3' ITR
<400> 10
aggaacccct agtgatggag ttggccactc cctctctgcg cgctcgctcg ctcactgagg 60
ccgggcgacc aaaggtcgcc cgacgcccgg gctttgcccg ggcggcctca gtgagcgagc 120
gagcgcgcag 130
<210> 11
<211> 2274
<212> DNA
<213> Artificial Sequence
<220>
<223> human Mfn2 engineered nucleic acid seuquence encoding mitofusin 2
protein
<400> 11
atgagcctgc tgttcagccg gtgcaacagc atcgtgaccg tgaagaaaaa caagcggcac 60
atggccgaag tgaacgcctc tccactgaag cacttcgtga ccgccaagaa gaagatcaac 120
ggcatcttcg agcagctggg cgcctacatc caagagagcg ccaccttcct ggaagatacc 180
tacagaaacg ccgagctgga ccccgtgacc acagaggaac aggtgctgga tgtgaagggc 240
tacctgagca aagtgcgggg catctctgaa gtgctggcca gacggcatat gaaggtggcc 300
tttttcggcc ggaccagcaa cggcaagagc accgtgatca atgccatgct gtgggacaaa 360
gtgctgccct ctggaatcgg ccacaccacc aactgctttc tgagagtgga aggcaccgac 420
ggccacgagg catttctgct gacagagggc tccgaggaaa agcggagcgc caagacagtg 480
aaccagctgg cccatgctct gcaccaggat aagcagctgc atgccggaag cctggtgtcc 540
gtgatgtggc ccaatagcaa gtgccctctg ctgaaggacg acctggtgct gatggatagc 600
cccgggatcg atgtgaccac cgaactggac agctggatcg acaagttctg cctggacgcc 660
gacgtgttcg tgctggtggc caatagcgag agcaccctga tgcagaccga gaagcacttt 720
ttccacaagg tgtccgagcg gctgagcaga cccaatatct ttatcctgaa caacagatgg 780
gacgccagcg ccagcgagcc cgagtatatg gaagaagtgc ggcggcagca tatggaacgg 840
tgcacatcct ttctggtgga cgagctgggc gtcgtggata gatctcaggc cggcgacaga 900
atcttctttg tgtccgccaa agaggtgctg aacgcccgga ttcagaaagc ccagggaatg 960
cctgaaggcg gaggtgcact ggccgaggga tttcaagtgc ggatgttcga gttccagaac 1020
ttcgagcgga gattcgagga gtgcatcagc cagagcgccg tcaagaccaa gttcgagcag 1080
cataccgtgc gggccaagca gattgccgaa gccgtcagac tgatcatgga cagcctgcat 1140
atggccgcca gagagcagca ggtctactgc gaggaaatgc gggaagagag acaggaccgg 1200
ctgaagttca tcgacaagca gctggaactg ctggcccagg actacaagct gcggatcaag 1260
cagatcaccg aagaggtgga aagacaggtg tccaccgcta tggccgagga aatcagacgg 1320
ctgagcgtgc tggtcgacga ctaccagatg gactttcacc cctctccagt ggtgctgaaa 1380
gtctacaaaa acgagctgca ccggcacatc gaggaaggcc tgggcagaaa catgagcgac 1440
agatgcagca ccgccatcac caatagcctg cagaccatgc agcaggacat gatcgacggc 1500
ctgaaacctc tgctgcctgt gtccgtcaga tcccagatcg atatgctggt gccccggcag 1560
tgctttagcc tgaactacga cctgaactgc gacaagctgt gcgccgattt ccaagaggac 1620
atcgagtttc acttcagcct cggctggaca atgctggtca acagatttct gggccccaag 1680
aacagcagac gggccctgat gggctacaac gatcaggtgc agaggcccat tcctctgaca 1740
cccgccaatc ctagcatgcc tccactgcct cagggcagcc tgacacaaga ggaattcatg 1800
gtgtctatgg tcaccggcct ggccagcctg accagcagaa catctatggg catcctggtc 1860
gtcggcggcg ttgtgtggaa agctgttggc tggcggctga tcgccctgag ctttggcctg 1920
tatggcctgc tgtacgtgta cgagagactg acctggacca ccaaggccaa agagcgggcc 1980
ttcaagcggc agtttgtgga acacgcctcc gagaaactgc agctggtgat cagctacacc 2040
ggcagcaatt gcagccacca ggtgcagcaa gagctgtccg gaacattcgc ccacctgtgt 2100
cagcaggtcg acgtgaccag agagaacctg gaacaagaga tcgccgccat gaataagaaa 2160
atcgaggtgc tcgactccct gcagagcaag gccaagctgc tgagaaacaa ggccggctgg 2220
ctggacagcg agctgaatat gttcacccac cagtacctgc agcctagccg ctaa 2274
<210> 12
<211> 2271
<212> DNA
<213> Artificial Sequence
<220>
<223> rMfn2 engineered nucleic acid sequence encoding mitofusin 2
protein
<400> 12
atgtctctgc tgttcagccg gtgcaacagc atcgtgaccg tgaagaaaga caagaggcac 60
atggccgaag tgaacgcctc tccactgaag cacttcgtga ccgccaagaa gaagatcaac 120
ggcatcttcg agcagctggg cgcctacatc caagagtctg ccggcttcct ggaagatacc 180
cacagaaaca ccgagctgga ccccgtgacc acagaggaac aggtgctgga cgtgaagggc 240
tacctgtcta aagtgcgggg catcagcgag gtgctggcta gaaggcatat gaaggtggcc 300
tttttcggca ggaccagcaa cggcaagagc accgtgatca acgccatgct gtgggacaaa 360
gtgctgcctt ctggcatcgg ccacaccacc aactgctttc tgagagtcgg cggcacagac 420
ggccacgagg cttttttgct gaccgagggc tccgaagaga agaaatccgt gaaaaccgtg 480
aaccagctgg cccacgctct gcaccaggat gaacaactgc acgccggaag cctggtgtcc 540
gtgatgtggc ctaacagcaa gtgccctctg ctgaaggacg acctggtgct gatggactct 600
cctggaatcg acgtgaccac tgagctggac agctggatcg acaagttctg cctggacgcc 660
gacgtgttcg tgctggtggc taactctgag agcaccctga tgcagaccga gaagcagttc 720
ttccacaagg tgtccgagag gctgagcagg cccaatatct ttatcctgaa caacagatgg 780
gacgccagcg ccagcgagcc cgagtatatg gaagaagtgc ggaggcagca tatggaaagg 840
tgtaccagct tcctggtgga cgagctggga gtcgtggata gagcacaggc cggcgacaga 900
atcttcttcg tgtctgccaa agaggtgctg agcgccaggg tgcagaaagc ccagggaatg 960
cctgaaggcg gcggagcttt ggccgaggga tttcaagtgc ggatgttcga gttccagaac 1020
ttcgagcgga gattcgagga atgcatcagc cagagcgccg tcaagacaaa gttcgagcag 1080
cacacagtgc gggccaagca gatcgctgag gctgtgcggc tgatcatgga cagcctgcat 1140
atcgccgctc aagagcagag ggtgtactgc ctggaaatgc gggaagagag gcaggacagg 1200
ctgagattca tcgacaagca gctggaactg ctggcccagg actacaagct gaggatcaag 1260
cagatgaccg aagaggtgga aagacaggtg tccaccgcca tggccgagga aatccgtaga 1320
ctgtctgtgc tggtcgacga gtaccagatg gactttcacc cctctccagt ggtgctgaag 1380
gtctacaaaa acgagctgca caggcacatc gaggaaggcc tgggcagaaa catgagcgac 1440
aggtgctcta ccgctatcgc cagcagcctg cagacaatgc agcaggacat gatcgacggc 1500
ctgaagcctc tgctgcctgt gtctgtgcgg aaccagatcg atatgctggt gcccaggcag 1560
tgcttctccc tgtcctacga cctgaactgc gacaagctgt gtgccgactt ccaagaggac 1620
atcgagtttc acttcagcct cggctggaca atgctggtca acagattcct gggacctaag 1680
aactccagac gggccctgct gggatacaac gatcaggtgc aaaggcccct gcctctgaca 1740
ccagctaacc cttctatgcc tcctctgcct caaggctctc tgacccaaga ggaactgatg 1800
gtgtccatgg tcacaggcct ggcttccctg accagcagaa cctctatggg catcctggtc 1860
gtcggcggag ttgtgtggaa agctgttggc tggcgcctga tcgccctgag ctttggactg 1920
tacggactgc tgtacgtgta cgagagactg acctggacca ccagggccaa agagagggcc 1980
ttcaagaggc agttcgtgga atacgcctcc gagaaactgc agctgattat ctcctacacc 2040
ggcagcaact gcagccacca ggtgcagcaa gagctgtctg gaacattcgc ccacctgtgc 2100
cagcaggtcg acatcaccag agacaacctg gaacaagaga tcgccgctat gaataagaag 2160
gtggaagccc tggactccct gcagagcaag gctaagctgc tgagaaacaa ggccggctgg 2220
ctggactccg agctgaatat gtttatccac cagtacctgc agcctagccg c 2271
<210> 13
<211> 23
<212> DNA
<213> Artificial Sequence
<220>
<223> 5'flank
<400> 13
ctggaggctt gctgaaggct gta 23
<210> 14
<211> 44
<212> DNA
<213> Artificial Sequence
<220>
<223> 3'flank
<400> 14
caggacacaa ggcctgttac tagcactcac atggaacaaa tggc 44
<210> 15
<211> 64
<212> DNA
<213> Artificial Sequence
<220>
<223> hMfn2 miR1693
<400> 15
tgctgttctt ataaaccttg aggactgttt tggccactga ctgacagtcc tcagtttata 60
agaa 64
<210> 16
<211> 64
<212> DNA
<213> Artificial Sequence
<220>
<223> rMfn2 miR1518
<400> 16
tgctgttctt ataaaccttg aggacagttt tggccactga ctgactgtcc tcagtttata 60
agaa 64
<210> 17
<211> 90
<212> DNA
<213> Artificial Sequence
<220>
<223> linker
<400> 17
tgtacaagta aagcgcccgc aggcttgcac ccgtaccttt gggagcgcgc gccctcgtcg 60
tgtcgtgacg tcacccgttc tgttggatcc 90
<210> 18
<211> 2274
<212> DNA
<213> Artificial Sequence
<220>
<223> hMfn2 endogenous nucleic acid sequence
<220>
<221> CDS
<222> (1)..(2274)
<400> 18
atg tcc ctg ctc ttc tct cga tgc aac tct atc gtc aca gtc aag aaa 48
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
aat aag aga cac atg gct gag gtg aat gca tcc cca ctt aag cac ttt 96
Asn Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
gtc act gcc aag aag aag atc aat ggc att ttt gag cag ctg ggg gcc 144
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
tac atc cag gag agc gcc acc ttc ctt gaa gac acg tac agg aat gca 192
Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala
50 55 60
gaa ctg gac ccc gtt acc aca gaa gaa cag gtt ctg gac gtc aaa ggt 240
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
tac cta tcc aaa gtg aga ggc atc agt gag gtg ctg gct cgg agg cac 288
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
atg aaa gtg gct ttt ttt ggc cgg acg agc aat ggg aag agc acc gtg 336
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
atc aat gcc atg ctc tgg gac aaa gtt ctg ccc tct ggg att ggc cac 384
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
acc acc aat tgc ttc ctg cgg gta gag ggc aca gat ggc cat gag gcc 432
Thr Thr Asn Cys Phe Leu Arg Val Glu Gly Thr Asp Gly His Glu Ala
130 135 140
ttt ctc ctt acc gag ggc tca gag gaa aag agg agt gcc aag act gtg 480
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Arg Ser Ala Lys Thr Val
145 150 155 160
aac cag ctg gcc cat gcc ctc cac cag gac aag cag ctc cat gcc ggc 528
Asn Gln Leu Ala His Ala Leu His Gln Asp Lys Gln Leu His Ala Gly
165 170 175
agc cta gtg agt gtg atg tgg ccc aac tct aag tgc cca ctt ctg aag 576
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
gat gac ctc gtt ttg atg gac agc cct ggt att gat gtc acc aca gag 624
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
ctg gac agc tgg att gac aag ttt tgt ctg gat gct gat gtg ttt gtg 672
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
ctg gtg gcc aac tca gag tcc acc ctg atg cag acg gaa aag cac ttc 720
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys His Phe
225 230 235 240
ttc cac aag gtg agt gag cgt ctc tcc cgg cca aac atc ttc atc ctg 768
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
aac aac cgc tgg gat gca tct gcc tca gag ccc gag tac atg gag gag 816
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
gtg cgg cgg cag cac atg gag cgt tgt acc agc ttc ctg gtg gat gag 864
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
ctg ggc gtg gtg gat cga tcc cag gcc ggg gac cgc atc ttc ttt gtg 912
Leu Gly Val Val Asp Arg Ser Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
tct gct aag gag gtg ctc aac gcc agg att cag aaa gcc cag ggc atg 960
Ser Ala Lys Glu Val Leu Asn Ala Arg Ile Gln Lys Ala Gln Gly Met
305 310 315 320
cct gaa gga ggg ggc gct ctc gca gaa ggc ttt caa gtg agg atg ttt 1008
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
gag ttt cag aat ttt gag agg aga ttt gag gag tgc atc tcc cag tct 1056
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
gca gtg aag acc aag ttt gag cag cac acg gtc cgg gcc aag cag att 1104
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
gca gag gcg gtt cga ctc atc atg gac tcc ctg cac atg gcg gct cgg 1152
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Met Ala Ala Arg
370 375 380
gag cag cag gtt tac tgc gag gaa atg cgt gaa gag cgg caa gac cga 1200
Glu Gln Gln Val Tyr Cys Glu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
ctg aaa ttt att gac aaa cag ctg gag ctc ttg gct caa gac tat aag 1248
Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
ctg cga att aag cag att acg gag gaa gtg gag agg cag gtg tcg act 1296
Leu Arg Ile Lys Gln Ile Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
gca atg gcc gag gag atc agg cgc ctc tct gta ctg gtg gac gat tac 1344
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Asp Tyr
435 440 445
cag atg gac ttc cac cct tct cca gta gtc ctc aag gtt tat aag aat 1392
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
gag ctg cac cgc cac ata gag gaa gga ctg ggt cga aac atg tct gac 1440
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
cgc tgc tcc acg gcc atc acc aac tcc ctg cag acc atg cag cag gac 1488
Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
atg ata gat ggc ttg aaa ccc ctc ctt cct gtg tct gtg cgg agt cag 1536
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Ser Gln
500 505 510
ata gac atg ctg gtc cca cgc cag tgc ttc tcc ctc aac tat gac cta 1584
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu
515 520 525
aac tgt gac aag ctg tgt gct gac ttc cag gaa gac att gag ttc cat 1632
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
ttc tct ctc gga tgg acc atg ctg gtg aat agg ttc ctg ggc ccc aag 1680
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
aac agc cgt cgg gcc ttg atg ggc tac aat gac cag gtc cag cgt ccc 1728
Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
atc cct ctg acg cca gcc aac ccc agc atg ccc cca ctg cca cag ggc 1776
Ile Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
tcg ctc acc cag gag gag ttc atg gtt tcc atg gtt acc ggc ctg gcc 1824
Ser Leu Thr Gln Glu Glu Phe Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
tcc ttg aca tcc agg acc tcc atg ggc att ctt gtt gtt gga gga gtg 1872
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
gtg tgg aag gca gtg ggc tgg cgg ctc att gcc ctc tcc ttt ggg ctc 1920
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
tat ggc ctc ctc tac gtc tat gag cgt ctg acc tgg acc acc aag gcc 1968
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala
645 650 655
aag gag agg gcc ttc aag cgc cag ttt gtg gag cat gcc agc gag aag 2016
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu His Ala Ser Glu Lys
660 665 670
ctg cag ctt gtc atc agc tac act ggc tcc aac tgc agc cac caa gtc 2064
Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
cag cag gaa ctg tct ggg acc ttt gct cat ctg tgt cag caa gtt gac 2112
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
gtc acc cgg gag aac ctg gag cag gaa att gcc gcc atg aac aag aaa 2160
Val Thr Arg Glu Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
att gag gtt ctt gac tca ctt cag agc aaa gca aag ctg ctc agg aat 2208
Ile Glu Val Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
aaa gcc ggt tgg ttg gac agt gag ctc aac atg ttc aca cac cag tac 2256
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Thr His Gln Tyr
740 745 750
ctg cag ccc agc aga tag 2274
Leu Gln Pro Ser Arg
755
<210> 19
<211> 757
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 19
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
Asn Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala
50 55 60
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
Thr Thr Asn Cys Phe Leu Arg Val Glu Gly Thr Asp Gly His Glu Ala
130 135 140
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Arg Ser Ala Lys Thr Val
145 150 155 160
Asn Gln Leu Ala His Ala Leu His Gln Asp Lys Gln Leu His Ala Gly
165 170 175
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys His Phe
225 230 235 240
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
Leu Gly Val Val Asp Arg Ser Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
Ser Ala Lys Glu Val Leu Asn Ala Arg Ile Gln Lys Ala Gln Gly Met
305 310 315 320
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Met Ala Ala Arg
370 375 380
Glu Gln Gln Val Tyr Cys Glu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
Leu Arg Ile Lys Gln Ile Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Asp Tyr
435 440 445
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Ser Gln
500 505 510
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu
515 520 525
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
Ile Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
Ser Leu Thr Gln Glu Glu Phe Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala
645 650 655
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu His Ala Ser Glu Lys
660 665 670
Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
Val Thr Arg Glu Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
Ile Glu Val Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Thr His Gln Tyr
740 745 750
Leu Gln Pro Ser Arg
755
<210> 20
<211> 2274
<212> DNA
<213> Artificial Sequence
<220>
<223> rMfn2 endogenous nucleic acid sequence
<220>
<221> CDS
<222> (1)..(2274)
<400> 20
atg tcc ctg ctc ttt tct cga tgc aac tcc atc gtc acc gtc aag aag 48
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
gat aag cga cac atg gct gag gtg aat gct tcc cct ctc aag cac ttt 96
Asp Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
gtc act gcc aag aaa aag atc aat ggc atc ttt gag cag ctg ggg gcc 144
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
tac atc caa gag agt gcc ggc ttc ctt gaa gac acc cac agg aat aca 192
Tyr Ile Gln Glu Ser Ala Gly Phe Leu Glu Asp Thr His Arg Asn Thr
50 55 60
gaa ctg gac cca gtt act aca gaa gag cag gtc ctg gat gtc aaa ggg 240
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
tac ctg tcc aag gtc agg gga atc agc gag gtg ctg gcc agg cgg cac 288
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
atg aag gtg gct ttt ttt ggc cgg acg agc aat ggg aag agc acc gtg 336
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
atc aat gcc atg ctt tgg gac aaa gtt ctg cca tct ggg att ggc cac 384
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
acc acc aat tgc ttc ctg cgg gtt ggg ggc acg gat ggc cac gag gcc 432
Thr Thr Asn Cys Phe Leu Arg Val Gly Gly Thr Asp Gly His Glu Ala
130 135 140
ttc ctc ctc acg gag ggc tca gaa gag aag aag agt gtc aag acc gtg 480
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Lys Ser Val Lys Thr Val
145 150 155 160
aac cag cta gcc cat gcc ctc cat cag gat gag cag ctg cat gca ggc 528
Asn Gln Leu Ala His Ala Leu His Gln Asp Glu Gln Leu His Ala Gly
165 170 175
agc ctg gtg agt gtg atg tgg ccc aac tcc aag tgt cca ctt ctg aag 576
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
gat gac ctc gtg ctg atg gac agc cct ggg atc gat gtc acc acg gag 624
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
ctg gac agc tgg att gat aag ttt tgc ctg gat gct gat gtg ttt gta 672
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
ctg gtg gcc aac tca gag tcc acg ctg atg cag acg gag aag cag ttc 720
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys Gln Phe
225 230 235 240
ttc cac aaa gtg agt gag cgt ctc tcc cgg ccc aac atc ttc atc ctg 768
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
aac aac cgc tgg gat gcg tct gcc tcg gag cct gag tac atg gag gag 816
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
gtg cgg cgg cag cac atg gaa cgc tgc acc agc ttt ctg gtg gat gag 864
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
cta ggc gtg gtg gat cga gct cag gcc ggg gac cgg atc ttc ttt gtg 912
Leu Gly Val Val Asp Arg Ala Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
tct gcc aag gag gtg ctc agt gcc agg gtc cag aaa gcc cag ggc atg 960
Ser Ala Lys Glu Val Leu Ser Ala Arg Val Gln Lys Ala Gln Gly Met
305 310 315 320
cca gaa gga ggt ggc gct ctt gca gaa ggt ttt caa gtg agg atg ttt 1008
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
gag ttt cag aat ttc gag agg cga ttt gag gag tgc att tcc cag tct 1056
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
gca gta aag acc aaa ttt gag cag cac aca gtc cgg gcc aag cag att 1104
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
gca gag gcc gtc cgt ctc atc atg gat tcc ctg cac att gcg gct cag 1152
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Ile Ala Ala Gln
370 375 380
gag cag cgg gtt tat tgt ctt gaa atg cgg gaa gag cgg caa gac cgg 1200
Glu Gln Arg Val Tyr Cys Leu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
ctg aga ttc att gac aag cag ctg gag ctc ctg gct caa gac tat aag 1248
Leu Arg Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
cta cgg att aag cag atg aca gag gaa gtg gaa agg cag gtg tcc aca 1296
Leu Arg Ile Lys Gln Met Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
gcc atg gct gaa gag atc agg cgc ctc tct gtg ctg gtt gac gag tac 1344
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Glu Tyr
435 440 445
cag atg gac ttt cac cca tcc cca gtt gtc ctc aag gtt tat aag aat 1392
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
gaa ctg cac cgc cat ata gag gaa ggc ctg gga cga aac atg tct gac 1440
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
cgc tgc tcc aca gcc att gcc agt tca ctg cag act atg cag caa gac 1488
Arg Cys Ser Thr Ala Ile Ala Ser Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
atg ata gac ggc ttg aag ccc ctt ctt cct gtg tct gtg cgg aat cag 1536
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Asn Gln
500 505 510
ata gac atg ctg gtc cct cga cag tgt ttc tcc ctc agc tat gac ctg 1584
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Ser Tyr Asp Leu
515 520 525
aac tgt gac aag ctg tgc gct gac ttt cag gag gac atc gaa ttc cat 1632
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
ttc tcc ctt gga tgg act atg cta gtg aat agg ttc ctg ggc cct aag 1680
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
aat agc cgg cgg gcc ttg ctg ggc tac aat gat cag gtt cag cgt cct 1728
Asn Ser Arg Arg Ala Leu Leu Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
ctc cct ctg aca cct gcc aac ccc agc atg cca ccc ttg cca cag ggc 1776
Leu Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
tcc ctc acc cag gag gag ctc atg gtc tcc atg gtt act ggc ctg gcc 1824
Ser Leu Thr Gln Glu Glu Leu Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
tct ctg act tcc agg acc tct atg ggc att ctc gtg gtc gga gga gtg 1872
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
gtg tgg aag gca gtg ggc tgg aga ctc atc gcc ctc tcc ttt gga ctg 1920
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
tat ggc ctc ctg tac gtg tat gag cgg ctg acc tgg acc acc aga gcc 1968
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Arg Ala
645 650 655
aag gag agg gcc ttc aag cgc cag ttt gtg gag tat gcc agt gag aag 2016
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu Tyr Ala Ser Glu Lys
660 665 670
ctg cag ctc att atc agt tat acc ggc tct aac tgc agc cac caa gtt 2064
Leu Gln Leu Ile Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
cag caa gaa ttg tct ggg aca ttt gct cat ctg tgc cag caa gtt gac 2112
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
atc acc cgg gat aat ctg gag cag gaa att gct gcc atg aac aag aaa 2160
Ile Thr Arg Asp Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
gtt gag gct ctg gat tca ctt cag agc aaa gcc aaa ttg ctc agg aat 2208
Val Glu Ala Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
aaa gct ggc tgg ttg gac agc gaa ctc aac atg ttc ata cac cag tac 2256
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Ile His Gln Tyr
740 745 750
ctg cag ccc agc aga tag 2274
Leu Gln Pro Ser Arg
755
<210> 21
<211> 757
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 21
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
Asp Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
Tyr Ile Gln Glu Ser Ala Gly Phe Leu Glu Asp Thr His Arg Asn Thr
50 55 60
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
Thr Thr Asn Cys Phe Leu Arg Val Gly Gly Thr Asp Gly His Glu Ala
130 135 140
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Lys Ser Val Lys Thr Val
145 150 155 160
Asn Gln Leu Ala His Ala Leu His Gln Asp Glu Gln Leu His Ala Gly
165 170 175
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys Gln Phe
225 230 235 240
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
Leu Gly Val Val Asp Arg Ala Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
Ser Ala Lys Glu Val Leu Ser Ala Arg Val Gln Lys Ala Gln Gly Met
305 310 315 320
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Ile Ala Ala Gln
370 375 380
Glu Gln Arg Val Tyr Cys Leu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
Leu Arg Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
Leu Arg Ile Lys Gln Met Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Glu Tyr
435 440 445
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
Arg Cys Ser Thr Ala Ile Ala Ser Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Asn Gln
500 505 510
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Ser Tyr Asp Leu
515 520 525
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
Asn Ser Arg Arg Ala Leu Leu Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
Leu Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
Ser Leu Thr Gln Glu Glu Leu Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Arg Ala
645 650 655
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu Tyr Ala Ser Glu Lys
660 665 670
Leu Gln Leu Ile Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
Ile Thr Arg Asp Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
Val Glu Ala Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Ile His Gln Tyr
740 745 750
Leu Gln Pro Ser Arg
755
<210> 22
<211> 215
<212> DNA
<213> Artificial Sequence
<220>
<223> bGH polyA
<400> 22
gcctcgactg tgccttctag ttgccagcca tctgttgttt gcccctcccc cgtgccttcc 60
ttgaccctgg aaggtgccac tcccactgtc ctttcctaat aaaatgagga aattgcatcg 120
cattgtctga gtaggtgtca ttctattctg gggggtgggg tggggcagga cagcaagggg 180
gaggattggg aagacaatag caggcatgct gggga 215
<210> 23
<211> 232
<212> DNA
<213> Artificial Sequence
<220>
<223> SV40 polyA
<400> 23
cgagcagaca tgataagata cattgatgag tttggacaaa ccacaactag aatgcagtga 60
aaaaaatgct ttatttgtga aatttgtgat gctattgctt tatttgtaac cattataagc 120
tgcaataaac aagttaacaa caacaattgc attcatttta tgtttcaggt tcagggggag 180
atgtgggagg ttttttaaag caagtaaaac ctctacaaat gtggtaaaat cg 232
<210> 24
<211> 2315
<212> DNA
<213> Artificial Sequence
<220>
<223> hMfn2 engineered nucleic acid sequnece V1
<220>
<221> CDS
<222> (1)..(2274)
<400> 24
gct agc acc ggt gcc acc atg agc ctg ctg ttc agc cgg tgc aac agc 48
Ala Ser Thr Gly Ala Thr Met Ser Leu Leu Phe Ser Arg Cys Asn Ser
1 5 10 15
atc gtg acc gtg aag aaa aac aag cgg cac atg gcc gaa gtg aac gcc 96
Ile Val Thr Val Lys Lys Asn Lys Arg His Met Ala Glu Val Asn Ala
20 25 30
tct cca ctg aag cac ttc gtg acc gcc aag aag aag atc aac ggc atc 144
Ser Pro Leu Lys His Phe Val Thr Ala Lys Lys Lys Ile Asn Gly Ile
35 40 45
ttc gag cag ctg ggc gcc tac atc caa gag agc gcc acc ttc ctg gaa 192
Phe Glu Gln Leu Gly Ala Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu
50 55 60
gat acc tac aga aac gcc gag ctg gac ccc gtg acc aca gag gaa cag 240
Asp Thr Tyr Arg Asn Ala Glu Leu Asp Pro Val Thr Thr Glu Glu Gln
65 70 75 80
gtg ctg gat gtg aag ggc tac ctg agc aaa gtg cgg ggc atc tct gaa 288
Val Leu Asp Val Lys Gly Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu
85 90 95
gtg ctg gcc aga cgg cat atg aag gtg gcc ttt ttc ggc cgg acc agc 336
Val Leu Ala Arg Arg His Met Lys Val Ala Phe Phe Gly Arg Thr Ser
100 105 110
aac ggc aag agc acc gtg atc aat gcc atg ctg tgg gac aaa gtg ctg 384
Asn Gly Lys Ser Thr Val Ile Asn Ala Met Leu Trp Asp Lys Val Leu
115 120 125
ccc tct gga atc ggc cac acc acc aac tgc ttt ctg aga gtg gaa ggc 432
Pro Ser Gly Ile Gly His Thr Thr Asn Cys Phe Leu Arg Val Glu Gly
130 135 140
acc gac ggc cac gag gca ttt ctg ctg aca gag ggc tcc gag gaa aag 480
Thr Asp Gly His Glu Ala Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys
145 150 155 160
cgg agc gcc aag aca gtg aac cag ctg gcc cat gct ctg cac cag gat 528
Arg Ser Ala Lys Thr Val Asn Gln Leu Ala His Ala Leu His Gln Asp
165 170 175
aag cag ctg cat gcc gga agc ctg gtg tcc gtg atg tgg ccc aat agc 576
Lys Gln Leu His Ala Gly Ser Leu Val Ser Val Met Trp Pro Asn Ser
180 185 190
aag tgc cct ctg ctg aag gac gac ctg gtg ctg atg gat agc ccc ggg 624
Lys Cys Pro Leu Leu Lys Asp Asp Leu Val Leu Met Asp Ser Pro Gly
195 200 205
atc gat gtg acc acc gaa ctg gac agc tgg atc gac aag ttc tgc ctg 672
Ile Asp Val Thr Thr Glu Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu
210 215 220
gac gcc gac gtg ttc gtg ctg gtg gcc aat agc gag agc acc ctg atg 720
Asp Ala Asp Val Phe Val Leu Val Ala Asn Ser Glu Ser Thr Leu Met
225 230 235 240
cag acc gag aag cac ttt ttc cac aag gtg tcc gag cgg ctg agc aga 768
Gln Thr Glu Lys His Phe Phe His Lys Val Ser Glu Arg Leu Ser Arg
245 250 255
ccc aac aat ttt atc ctg aac aac aga tgg gac gcc agc gcc agc gag 816
Pro Asn Asn Phe Ile Leu Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu
260 265 270
ccc gag tat atg gaa gaa gtg cgg cgg cag cat atg gaa cgg tgc aca 864
Pro Glu Tyr Met Glu Glu Val Arg Arg Gln His Met Glu Arg Cys Thr
275 280 285
tcc ttt ctg gtg gac gag ctg ggc gtc gtg gat aga tct cag gcc ggc 912
Ser Phe Leu Val Asp Glu Leu Gly Val Val Asp Arg Ser Gln Ala Gly
290 295 300
gac aga atc ttc ttt gtg tcc gcc aaa gag gtg ctg aac gcc cgg att 960
Asp Arg Ile Phe Phe Val Ser Ala Lys Glu Val Leu Asn Ala Arg Ile
305 310 315 320
cag aaa gcc cag gga atg cct gaa ggc gga ggt gca ctg gcc gag gga 1008
Gln Lys Ala Gln Gly Met Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly
325 330 335
ttt caa gtg cgg atg ttc gag ttc cag aac ttc gag cgg aga ttc gag 1056
Phe Gln Val Arg Met Phe Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu
340 345 350
gaa tgc atc agc cag agc gcc gtc aag acc aag ttt gag cag cat acc 1104
Glu Cys Ile Ser Gln Ser Ala Val Lys Thr Lys Phe Glu Gln His Thr
355 360 365
gtg cgg gcc aag cag att gcc gaa gcc gtc aga ctg atc atg gac agc 1152
Val Arg Ala Lys Gln Ile Ala Glu Ala Val Arg Leu Ile Met Asp Ser
370 375 380
ctg cat atg gcc gcc aga gag cag cag gtc tac tgc gag gaa atg cgg 1200
Leu His Met Ala Ala Arg Glu Gln Gln Val Tyr Cys Glu Glu Met Arg
385 390 395 400
gaa gag aga cag gac cgg ctg aag ttc atc gac aag cag ctg gaa ctg 1248
Glu Glu Arg Gln Asp Arg Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu
405 410 415
ctg gcc cag gac tac aag ctg cgg atc aag cag atc acc gaa gag gtg 1296
Leu Ala Gln Asp Tyr Lys Leu Arg Ile Lys Gln Ile Thr Glu Glu Val
420 425 430
gaa aga cag gtg tcc acc gct atg gcc gag gaa atc aga cgg ctg agc 1344
Glu Arg Gln Val Ser Thr Ala Met Ala Glu Glu Ile Arg Arg Leu Ser
435 440 445
gtg ctg gtc gac gac tac cag atg gac ttt cac ccc tct cca gtg gtg 1392
Val Leu Val Asp Asp Tyr Gln Met Asp Phe His Pro Ser Pro Val Val
450 455 460
ctg aag gtc tac aag aac gag ctg cac cgg cac atc gag gaa ggc ctg 1440
Leu Lys Val Tyr Lys Asn Glu Leu His Arg His Ile Glu Glu Gly Leu
465 470 475 480
ggc aga aac atg agc gac aga tgc agc acc gcc atc acc aat agc ctg 1488
Gly Arg Asn Met Ser Asp Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu
485 490 495
cag acc atg cag cag gac atg atc gac ggc ctg aaa cct ctg ctg cct 1536
Gln Thr Met Gln Gln Asp Met Ile Asp Gly Leu Lys Pro Leu Leu Pro
500 505 510
gtg tcc gtc aga tcc cag atc gat atg ctg gtg ccc cgg cag tgc ttt 1584
Val Ser Val Arg Ser Gln Ile Asp Met Leu Val Pro Arg Gln Cys Phe
515 520 525
agc ctg aac tac gac ctg aac tgc gac aag ctg tgc gcc gat ttc caa 1632
Ser Leu Asn Tyr Asp Leu Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln
530 535 540
gag gac atc gag ttt cac ttc agc ctc ggc tgg aca atg ctg gtc aac 1680
Glu Asp Ile Glu Phe His Phe Ser Leu Gly Trp Thr Met Leu Val Asn
545 550 555 560
aga ttt ctg ggc ccc aag aac agc aga cgg gcc ctg atg ggc tac aac 1728
Arg Phe Leu Gly Pro Lys Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn
565 570 575
gat cag gtg cag agg ccc att cct ctg aca ccc gcc aat cct agc atg 1776
Asp Gln Val Gln Arg Pro Ile Pro Leu Thr Pro Ala Asn Pro Ser Met
580 585 590
cct cca ctg cct cag ggc agc ctg aca caa gag gaa ttc atg gtg tct 1824
Pro Pro Leu Pro Gln Gly Ser Leu Thr Gln Glu Glu Phe Met Val Ser
595 600 605
atg gtc acc ggc ctg gcc agc ctg acc agc aga aca tct atg ggc atc 1872
Met Val Thr Gly Leu Ala Ser Leu Thr Ser Arg Thr Ser Met Gly Ile
610 615 620
ctg gtc gtc ggc ggc gtt gtg tgg aaa gct gtt ggc tgg cgg ctg atc 1920
Leu Val Val Gly Gly Val Val Trp Lys Ala Val Gly Trp Arg Leu Ile
625 630 635 640
gcc ctg agc ttt ggc ctg tat ggc ctg ctg tac gtg tac gag aga ctg 1968
Ala Leu Ser Phe Gly Leu Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu
645 650 655
acc tgg acc acc aag gcc aaa gag cgg gcc ttc aag cgg cag ttt gtg 2016
Thr Trp Thr Thr Lys Ala Lys Glu Arg Ala Phe Lys Arg Gln Phe Val
660 665 670
gaa cac gcc tcc gag aaa ctg cag ctg gtg atc agc tac acc ggc agc 2064
Glu His Ala Ser Glu Lys Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser
675 680 685
aat tgc agc cac cag gtg cag caa gag ctg tcc gga aca ttc gcc cac 2112
Asn Cys Ser His Gln Val Gln Gln Glu Leu Ser Gly Thr Phe Ala His
690 695 700
ctg tgt cag cag gtc gac gtg acc aga gag aac ctg gaa caa gag atc 2160
Leu Cys Gln Gln Val Asp Val Thr Arg Glu Asn Leu Glu Gln Glu Ile
705 710 715 720
gcc gcc atg aac aag aaa atc gag gtg ctc gac tcc ctg cag agc aag 2208
Ala Ala Met Asn Lys Lys Ile Glu Val Leu Asp Ser Leu Gln Ser Lys
725 730 735
gcc aag ctg ctg aga aac aag gcc ggc tgg ctg gac agc gag ctg aat 2256
Ala Lys Leu Leu Arg Asn Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn
740 745 750
atg ttc acc cac cag tac ctgcagccta gccgctaata atgtacagcg 2304
Met Phe Thr His Gln Tyr
755
gccgcaagct t 2315
<210> 25
<211> 758
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 25
Ala Ser Thr Gly Ala Thr Met Ser Leu Leu Phe Ser Arg Cys Asn Ser
1 5 10 15
Ile Val Thr Val Lys Lys Asn Lys Arg His Met Ala Glu Val Asn Ala
20 25 30
Ser Pro Leu Lys His Phe Val Thr Ala Lys Lys Lys Ile Asn Gly Ile
35 40 45
Phe Glu Gln Leu Gly Ala Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu
50 55 60
Asp Thr Tyr Arg Asn Ala Glu Leu Asp Pro Val Thr Thr Glu Glu Gln
65 70 75 80
Val Leu Asp Val Lys Gly Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu
85 90 95
Val Leu Ala Arg Arg His Met Lys Val Ala Phe Phe Gly Arg Thr Ser
100 105 110
Asn Gly Lys Ser Thr Val Ile Asn Ala Met Leu Trp Asp Lys Val Leu
115 120 125
Pro Ser Gly Ile Gly His Thr Thr Asn Cys Phe Leu Arg Val Glu Gly
130 135 140
Thr Asp Gly His Glu Ala Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys
145 150 155 160
Arg Ser Ala Lys Thr Val Asn Gln Leu Ala His Ala Leu His Gln Asp
165 170 175
Lys Gln Leu His Ala Gly Ser Leu Val Ser Val Met Trp Pro Asn Ser
180 185 190
Lys Cys Pro Leu Leu Lys Asp Asp Leu Val Leu Met Asp Ser Pro Gly
195 200 205
Ile Asp Val Thr Thr Glu Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu
210 215 220
Asp Ala Asp Val Phe Val Leu Val Ala Asn Ser Glu Ser Thr Leu Met
225 230 235 240
Gln Thr Glu Lys His Phe Phe His Lys Val Ser Glu Arg Leu Ser Arg
245 250 255
Pro Asn Asn Phe Ile Leu Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu
260 265 270
Pro Glu Tyr Met Glu Glu Val Arg Arg Gln His Met Glu Arg Cys Thr
275 280 285
Ser Phe Leu Val Asp Glu Leu Gly Val Val Asp Arg Ser Gln Ala Gly
290 295 300
Asp Arg Ile Phe Phe Val Ser Ala Lys Glu Val Leu Asn Ala Arg Ile
305 310 315 320
Gln Lys Ala Gln Gly Met Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly
325 330 335
Phe Gln Val Arg Met Phe Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu
340 345 350
Glu Cys Ile Ser Gln Ser Ala Val Lys Thr Lys Phe Glu Gln His Thr
355 360 365
Val Arg Ala Lys Gln Ile Ala Glu Ala Val Arg Leu Ile Met Asp Ser
370 375 380
Leu His Met Ala Ala Arg Glu Gln Gln Val Tyr Cys Glu Glu Met Arg
385 390 395 400
Glu Glu Arg Gln Asp Arg Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu
405 410 415
Leu Ala Gln Asp Tyr Lys Leu Arg Ile Lys Gln Ile Thr Glu Glu Val
420 425 430
Glu Arg Gln Val Ser Thr Ala Met Ala Glu Glu Ile Arg Arg Leu Ser
435 440 445
Val Leu Val Asp Asp Tyr Gln Met Asp Phe His Pro Ser Pro Val Val
450 455 460
Leu Lys Val Tyr Lys Asn Glu Leu His Arg His Ile Glu Glu Gly Leu
465 470 475 480
Gly Arg Asn Met Ser Asp Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu
485 490 495
Gln Thr Met Gln Gln Asp Met Ile Asp Gly Leu Lys Pro Leu Leu Pro
500 505 510
Val Ser Val Arg Ser Gln Ile Asp Met Leu Val Pro Arg Gln Cys Phe
515 520 525
Ser Leu Asn Tyr Asp Leu Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln
530 535 540
Glu Asp Ile Glu Phe His Phe Ser Leu Gly Trp Thr Met Leu Val Asn
545 550 555 560
Arg Phe Leu Gly Pro Lys Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn
565 570 575
Asp Gln Val Gln Arg Pro Ile Pro Leu Thr Pro Ala Asn Pro Ser Met
580 585 590
Pro Pro Leu Pro Gln Gly Ser Leu Thr Gln Glu Glu Phe Met Val Ser
595 600 605
Met Val Thr Gly Leu Ala Ser Leu Thr Ser Arg Thr Ser Met Gly Ile
610 615 620
Leu Val Val Gly Gly Val Val Trp Lys Ala Val Gly Trp Arg Leu Ile
625 630 635 640
Ala Leu Ser Phe Gly Leu Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu
645 650 655
Thr Trp Thr Thr Lys Ala Lys Glu Arg Ala Phe Lys Arg Gln Phe Val
660 665 670
Glu His Ala Ser Glu Lys Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser
675 680 685
Asn Cys Ser His Gln Val Gln Gln Glu Leu Ser Gly Thr Phe Ala His
690 695 700
Leu Cys Gln Gln Val Asp Val Thr Arg Glu Asn Leu Glu Gln Glu Ile
705 710 715 720
Ala Ala Met Asn Lys Lys Ile Glu Val Leu Asp Ser Leu Gln Ser Lys
725 730 735
Ala Lys Leu Leu Arg Asn Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn
740 745 750
Met Phe Thr His Gln Tyr
755
<210> 26
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 26
aaaccttgag gactactgga g 21
<210> 27
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 27
ttgacgtcca gaacctgttc t 21
<210> 28
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 28
agaagtgggc acttagagtt g 21
<210> 29
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 29
ttcagaagtg ggcacttaga g 21
<210> 30
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 30
ttgtcaatcc agctgtccag c 21
<210> 31
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 31
caaacttggt cttcactgca g 21
<210> 32
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 32
aaaccttgag gactactgga g 21
<210> 33
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 33
taaccatgga aaccatgaac t 21
<210> 34
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 34
acaacaagaa tgcccatgga g 21
<210> 35
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 35
aaaggtccca gacagttcct g 21
<210> 36
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 36
tgttcatggc ggcaatttcc t 21
<210> 37
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 37
tgaggttggc tattgattga c 21
<210> 38
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 38
ttctcacaca gtcaacacct t 21
<210> 39
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 39
tttcctcgca gtaaacctgc t 21
<210> 40
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 40
agaaatggaa ctcaatgtct t 21
<210> 41
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 41
tgaacaggac atcacctgtg a 21
<210> 42
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 42
aatacaagca ggtatgtgaa c 21
<210> 43
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 43
taaacctgct gctcccgagc c 21
<210> 44
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 44
tagaggaggc catagagccc a 21
<210> 45
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 45
tctacccgca ggaagcaatt g 21
<210> 46
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> antisense sequence
<400> 46
ctccttagca gacacaaaga a 21
<210> 47
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 47
agaacaggtt ctggacgtca a 21
<210> 48
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 48
caactctaag tgcccacttc t 21
<210> 49
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 49
ctctaagtgc ccacttctga a 21
<210> 50
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 50
gctggacagc tggattgaca a 21
<210> 51
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 51
ctgcagtgaa gaccaagttt g 21
<210> 52
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 52
ctccagtagt cctcaaggtt t 21
<210> 53
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 53
agttcatggt ttccatggtt a 21
<210> 54
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 54
ctccatgggc attcttgttg t 21
<210> 55
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 55
caggaactgt ctgggacctt t 21
<210> 56
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 56
aggaaattgc cgccatgaac a 21
<210> 57
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 57
agtcctcaag gtttataaga a 21
<210> 58
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 58
gtcaatcaat agccaacctc a 21
<210> 59
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 59
aaggtgttga ctgtgtgaga a 21
<210> 60
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 60
agcaggttta ctgcgaggaa a 21
<210> 61
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 61
aagacattga gttccatttc t 21
<210> 62
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 62
tcacaggtga tgtcctgttc a 21
<210> 63
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 63
gttcacatac ctgcttgtat t 21
<210> 64
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 64
ggctcgggag cagcaggttt a 21
<210> 65
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 65
tgggctctat ggcctcctct a 21
<210> 66
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 66
caattgcttc ctgcgggtag a 21
<210> 67
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> Target hMfn2 Sequence
<400> 67
ttctttgtgt ctgctaagga g 21
<210> 68
<211> 21
<212> DNA
<213> Artificial Sequence
<220>
<223> miR1693(21-mer)
<400> 68
ttcttataaa ccttgaggac t 21
<210> 69
<211> 4771
<212> DNA
<213> Artificial Sequence
<220>
<223> Vector genome CAG.CI.hMfn2.GA.link.miR538.WPRE.SV40
<220>
<221> repeat_region
<222> (1)..(188)
<223> 5'ITR
<220>
<221> misc_feature
<222> (192)..(1032)
<223> CAG(CBA)
<220>
<221> enhancer
<222> (194)..(436)
<223> CMV enhancer
<220>
<221> promoter
<222> (439)..(720)
<223> CB promoter
<220>
<221> Intron
<222> (720)..(1127)
<223> Hybrid Intron in CAG
<220>
<221> Intron
<222> (720)..(950)
<223> b-actin intron
<220>
<221> misc_feature
<222> (1158)..(1163)
<223> Kozak
<220>
<221> CDS
<222> (1164)..(3437)
<223> human Mfn2 engineered
<220>
<221> misc_feature
<222> (1379)..(1399)
<223> miR538 mut
<220>
<221> misc_feature
<222> (2534)..(2554)
<223> miR1518 mutated
<220>
<221> misc_feature
<222> (3438)..(3519)
<223> linker p4271
<220>
<221> misc_feature
<222> (3520)..(3547)
<223> miR538 AS
<220>
<221> misc_feature
<222> (3569)..(3587)
<223> loop
<220>
<221> misc_feature
<222> (3588)..(3606)
<223> miR538 sense
<220>
<221> misc_feature
<222> (3607)..(3651)
<223> 3' flank
<220>
<221> misc_feature
<222> (3678)..(4266)
<223> WRPE
<220>
<221> misc_feature
<222> (4355)..(4474)
<223> SV40 PA temrinator
<220>
<221> repeat_region
<222> (4584)..(4771)
<223> 3'ITR
<400> 69
gctgcgcgct cgctcgctca ctgaggccgc ccgggcaaag cccgggcgtc gggcgacctt 60
tggtcgcccg gcctcagtga gcgagcgagc gcgcagagag ggagtggcca actccatcac 120
taggggttcc ttgtagttaa tgattaaccc gccatgctac ttatctacgt agccatgctc 180
taggaagagt accattgacg tcaataatga cgtatgttcc catagtaacg ccaataggga 240
ctttccattg acgtcaatgg gtggagtatt tacggtaaac tgcccacttg gcagtacatc 300
aagtgtatca tatgccaagt acgcccccta ttgacgtcaa tgacggtaaa tggcccgcct 360
ggcattatgc ccagtacatg accttatggg actttcctac ttggcagtac atctacgtat 420
tagtcatcgc tattaccatg gtcgaggtga gccccacgtt ctgcttcact ctccccatct 480
cccccccctc cccaccccca attttgtatt tatttatttt ttaattattt tgtgcagcga 540
tgggggcggg gggggggggg gggcgcgcgc caggcggggc ggggcggggc gaggggcggg 600
gcggggcgag gcggagaggt gcggcggcag ccaatcagag cggcgcgctc cgaaagtttc 660
cttttatggc gaggcggcgg cggcggcggc cctataaaaa gcgaagcgcg cggcgggcgg 720
gagtcgctgc gcgctgcctt cgccccgtgc cccgctccgc cgccgcctcg cgccgcccgc 780
cccggctctg actgaccgcg ttactcccac aggtgagcgg gcgggacggc ccttctcctc 840
cgggctgtaa ttagcgcttg gtttaatgac ggcttgtttc ttttctgtgg ctgcgtgaaa 900
gccttgaggg gctccgggag ggccctttgt gcggggggag cggctcgggg ctgtccgcgg 960
ggggacggct gccttcgggg gggacggggc agggcggggt tcggcttctg gcgtgtgacc 1020
ggcggctcta gagcctctgc taaccatgtt catgccttct tctttttcct acagctcctg 1080
ggcaacgtgc tggttattgt gctgtctcat cattttggca aagaattgga tcccgtacga 1140
cgcgtgctag caccggtgcc acc atg agc ctg ctg ttc agc cgg tgc aac agc 1193
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser
1 5 10
atc gtg acc gtg aag aaa aac aag cgg cac atg gcc gaa gtg aac gcc 1241
Ile Val Thr Val Lys Lys Asn Lys Arg His Met Ala Glu Val Asn Ala
15 20 25
tct cca ctg aag cac ttc gtg acc gcc aag aag aag atc aac ggc atc 1289
Ser Pro Leu Lys His Phe Val Thr Ala Lys Lys Lys Ile Asn Gly Ile
30 35 40
ttc gag cag ctg ggc gcc tac atc caa gag agc gcc acc ttc ctg gaa 1337
Phe Glu Gln Leu Gly Ala Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu
45 50 55
gat acc tac aga aac gcc gag ctg gac ccc gtg acc aca gag gaa cag 1385
Asp Thr Tyr Arg Asn Ala Glu Leu Asp Pro Val Thr Thr Glu Glu Gln
60 65 70
gtg ctg gat gtg aag ggc tac ctg agc aaa gtg cgg ggc atc tct gaa 1433
Val Leu Asp Val Lys Gly Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu
75 80 85 90
gtg ctg gcc aga cgg cat atg aag gtg gcc ttt ttc ggc cgg acc agc 1481
Val Leu Ala Arg Arg His Met Lys Val Ala Phe Phe Gly Arg Thr Ser
95 100 105
aac ggc aag agc acc gtg atc aat gcc atg ctg tgg gac aaa gtg ctg 1529
Asn Gly Lys Ser Thr Val Ile Asn Ala Met Leu Trp Asp Lys Val Leu
110 115 120
ccc tct gga atc ggc cac acc acc aac tgc ttt ctg aga gtg gaa ggc 1577
Pro Ser Gly Ile Gly His Thr Thr Asn Cys Phe Leu Arg Val Glu Gly
125 130 135
acc gac ggc cac gag gca ttt ctg ctg aca gag ggc tcc gag gaa aag 1625
Thr Asp Gly His Glu Ala Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys
140 145 150
cgg agc gcc aag aca gtg aac cag ctg gcc cat gct ctg cac cag gat 1673
Arg Ser Ala Lys Thr Val Asn Gln Leu Ala His Ala Leu His Gln Asp
155 160 165 170
aag cag ctg cat gcc gga agc ctg gtg tcc gtg atg tgg ccc aat agc 1721
Lys Gln Leu His Ala Gly Ser Leu Val Ser Val Met Trp Pro Asn Ser
175 180 185
aag tgc cct ctg ctg aag gac gac ctg gtg ctg atg gat agc ccc ggg 1769
Lys Cys Pro Leu Leu Lys Asp Asp Leu Val Leu Met Asp Ser Pro Gly
190 195 200
atc gat gtg acc acc gaa ctg gac agc tgg atc gac aag ttc tgc ctg 1817
Ile Asp Val Thr Thr Glu Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu
205 210 215
gac gcc gac gtg ttc gtg ctg gtg gcc aat agc gag agc acc ctg atg 1865
Asp Ala Asp Val Phe Val Leu Val Ala Asn Ser Glu Ser Thr Leu Met
220 225 230
cag acc gag aag cac ttt ttc cac aag gtg tcc gag cgg ctg agc aga 1913
Gln Thr Glu Lys His Phe Phe His Lys Val Ser Glu Arg Leu Ser Arg
235 240 245 250
ccc aat atc ttt atc ctg aac aac aga tgg gac gcc agc gcc agc gag 1961
Pro Asn Ile Phe Ile Leu Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu
255 260 265
ccc gag tat atg gaa gaa gtg cgg cgg cag cat atg gaa cgg tgc aca 2009
Pro Glu Tyr Met Glu Glu Val Arg Arg Gln His Met Glu Arg Cys Thr
270 275 280
tcc ttt ctg gtg gac gag ctg ggc gtc gtg gat aga tct cag gcc ggc 2057
Ser Phe Leu Val Asp Glu Leu Gly Val Val Asp Arg Ser Gln Ala Gly
285 290 295
gac aga atc ttc ttt gtg tcc gcc aaa gag gtg ctg aac gcc cgg att 2105
Asp Arg Ile Phe Phe Val Ser Ala Lys Glu Val Leu Asn Ala Arg Ile
300 305 310
cag aaa gcc cag gga atg cct gaa ggc gga ggt gca ctg gcc gag gga 2153
Gln Lys Ala Gln Gly Met Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly
315 320 325 330
ttt caa gtg cgg atg ttc gag ttc cag aac ttc gag cgg aga ttc gag 2201
Phe Gln Val Arg Met Phe Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu
335 340 345
gag tgc atc agc cag agc gcc gtc aag acc aag ttc gag cag cat acc 2249
Glu Cys Ile Ser Gln Ser Ala Val Lys Thr Lys Phe Glu Gln His Thr
350 355 360
gtg cgg gcc aag cag att gcc gaa gcc gtc aga ctg atc atg gac agc 2297
Val Arg Ala Lys Gln Ile Ala Glu Ala Val Arg Leu Ile Met Asp Ser
365 370 375
ctg cat atg gcc gcc aga gag cag cag gtc tac tgc gag gaa atg cgg 2345
Leu His Met Ala Ala Arg Glu Gln Gln Val Tyr Cys Glu Glu Met Arg
380 385 390
gaa gag aga cag gac cgg ctg aag ttc atc gac aag cag ctg gaa ctg 2393
Glu Glu Arg Gln Asp Arg Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu
395 400 405 410
ctg gcc cag gac tac aag ctg cgg atc aag cag atc acc gaa gag gtg 2441
Leu Ala Gln Asp Tyr Lys Leu Arg Ile Lys Gln Ile Thr Glu Glu Val
415 420 425
gaa aga cag gtg tcc acc gct atg gcc gag gaa atc aga cgg ctg agc 2489
Glu Arg Gln Val Ser Thr Ala Met Ala Glu Glu Ile Arg Arg Leu Ser
430 435 440
gtg ctg gtc gac gac tac cag atg gac ttt cac ccc tct cca gtg gtg 2537
Val Leu Val Asp Asp Tyr Gln Met Asp Phe His Pro Ser Pro Val Val
445 450 455
ctg aaa gtc tac aaa aac gag ctg cac cgg cac atc gag gaa ggc ctg 2585
Leu Lys Val Tyr Lys Asn Glu Leu His Arg His Ile Glu Glu Gly Leu
460 465 470
ggc aga aac atg agc gac aga tgc agc acc gcc atc acc aat agc ctg 2633
Gly Arg Asn Met Ser Asp Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu
475 480 485 490
cag acc atg cag cag gac atg atc gac ggc ctg aaa cct ctg ctg cct 2681
Gln Thr Met Gln Gln Asp Met Ile Asp Gly Leu Lys Pro Leu Leu Pro
495 500 505
gtg tcc gtc aga tcc cag atc gat atg ctg gtg ccc cgg cag tgc ttt 2729
Val Ser Val Arg Ser Gln Ile Asp Met Leu Val Pro Arg Gln Cys Phe
510 515 520
agc ctg aac tac gac ctg aac tgc gac aag ctg tgc gcc gat ttc caa 2777
Ser Leu Asn Tyr Asp Leu Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln
525 530 535
gag gac atc gag ttt cac ttc agc ctc ggc tgg aca atg ctg gtc aac 2825
Glu Asp Ile Glu Phe His Phe Ser Leu Gly Trp Thr Met Leu Val Asn
540 545 550
aga ttt ctg ggc ccc aag aac agc aga cgg gcc ctg atg ggc tac aac 2873
Arg Phe Leu Gly Pro Lys Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn
555 560 565 570
gat cag gtg cag agg ccc att cct ctg aca ccc gcc aat cct agc atg 2921
Asp Gln Val Gln Arg Pro Ile Pro Leu Thr Pro Ala Asn Pro Ser Met
575 580 585
cct cca ctg cct cag ggc agc ctg aca caa gag gaa ttc atg gtg tct 2969
Pro Pro Leu Pro Gln Gly Ser Leu Thr Gln Glu Glu Phe Met Val Ser
590 595 600
atg gtc acc ggc ctg gcc agc ctg acc agc aga aca tct atg ggc atc 3017
Met Val Thr Gly Leu Ala Ser Leu Thr Ser Arg Thr Ser Met Gly Ile
605 610 615
ctg gtc gtc ggc ggc gtt gtg tgg aaa gct gtt ggc tgg cgg ctg atc 3065
Leu Val Val Gly Gly Val Val Trp Lys Ala Val Gly Trp Arg Leu Ile
620 625 630
gcc ctg agc ttt ggc ctg tat ggc ctg ctg tac gtg tac gag aga ctg 3113
Ala Leu Ser Phe Gly Leu Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu
635 640 645 650
acc tgg acc acc aag gcc aaa gag cgg gcc ttc aag cgg cag ttt gtg 3161
Thr Trp Thr Thr Lys Ala Lys Glu Arg Ala Phe Lys Arg Gln Phe Val
655 660 665
gaa cac gcc tcc gag aaa ctg cag ctg gtg atc agc tac acc ggc agc 3209
Glu His Ala Ser Glu Lys Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser
670 675 680
aat tgc agc cac cag gtg cag caa gag ctg tcc gga aca ttc gcc cac 3257
Asn Cys Ser His Gln Val Gln Gln Glu Leu Ser Gly Thr Phe Ala His
685 690 695
ctg tgt cag cag gtc gac gtg acc aga gag aac ctg gaa caa gag atc 3305
Leu Cys Gln Gln Val Asp Val Thr Arg Glu Asn Leu Glu Gln Glu Ile
700 705 710
gcc gcc atg aat aag aaa atc gag gtg ctc gac tcc ctg cag agc aag 3353
Ala Ala Met Asn Lys Lys Ile Glu Val Leu Asp Ser Leu Gln Ser Lys
715 720 725 730
gcc aag ctg ctg aga aac aag gcc ggc tgg ctg gac agc gag ctg aat 3401
Ala Lys Leu Leu Arg Asn Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn
735 740 745
atg ttc acc cac cag tac ctg cag cct agc cgc taa taaagcggcc 3447
Met Phe Thr His Gln Tyr Leu Gln Pro Ser Arg
750 755
gcaagcttgc acccgtacct ttgggagcgc gcgccctcgt cgtgtcgtga cgtcacccgt 3507
tctgttggat ccctggaggc ttgctgaagg ctgtatgctg ttgacgtcca gaacctgttc 3567
tgttttggcc actgactgac agaacaggct ggacgtcaac aggacacaag gcctgttact 3627
agcactcaca tggaacaaat ggcccagatc ttaagcttct cgagatcgat aatcaacctc 3687
tggattacaa aatttgtgaa agattgactg gtattcttaa ctatgttgct ccttttacgc 3747
tatgtggata cgctgcttta atgcctttgt atcatgctat tgcttcccgt atggctttca 3807
ttttctcctc cttgtataaa tcctggttgc tgtctcttta tgaggagttg tggcccgttg 3867
tcaggcaacg tggcgtggtg tgcactgtgt ttgctgacgc aacccccact ggttggggca 3927
ttgccaccac ctgtcagctc ctttccggga ctttcgcttt ccccctccct attgccacgg 3987
cggaactcat cgccgcctgc cttgcccgct gctggacagg ggctcggctg ttgggcactg 4047
acaattccgt ggtgttgtcg gggaaatcat cgtcctttcc ttggctgctc gcctgtgttg 4107
ccacctggat tctgcgcggg acgcccttct gctacgtccc ttcggccctc aatccagcgg 4167
accttccttc ccgcggcctg ctgccggctc tgcggcctct tccgcgtctt cgccttcgcc 4227
ctcagacgag tcggatctcc ctttgggccg cctccccgcc tgctgatcgc cctgagcctg 4287
gccctggtga ccaacagcca ggtgcaattg ctagagtcga ctctagagcg gccgcttcga 4347
gcagacatga taagatacat tgatgagttt ggacaaacca caactagaat gcagtgaaaa 4407
aaatgcttta tttgtgaaat ttgtgatgct attgctttat ttgtaaccat tataagctgc 4467
aataaacaag ttaacaacaa caattgcatt cattttatgt ttcaggttca gggggagatg 4527
tgggaggttt tttaaagcaa gtaaaacctc tacaaatgtg gtaaaatcga taaggatctt 4587
cctagagcat ggctacgtag ataagtagca tggcgggtta atcattaact acaaggaacc 4647
cctagtgatg gagttggcca ctccctctct gcgcgctcgc tcgctcactg aggccgggcg 4707
accaaaggtc gcccgacgcc cgggctttgc ccgggcggcc tcagtgagcg agcgagcgcg 4767
cagc 4771
<210> 70
<211> 757
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 70
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
Asn Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala
50 55 60
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
Thr Thr Asn Cys Phe Leu Arg Val Glu Gly Thr Asp Gly His Glu Ala
130 135 140
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Arg Ser Ala Lys Thr Val
145 150 155 160
Asn Gln Leu Ala His Ala Leu His Gln Asp Lys Gln Leu His Ala Gly
165 170 175
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys His Phe
225 230 235 240
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
Leu Gly Val Val Asp Arg Ser Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
Ser Ala Lys Glu Val Leu Asn Ala Arg Ile Gln Lys Ala Gln Gly Met
305 310 315 320
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Met Ala Ala Arg
370 375 380
Glu Gln Gln Val Tyr Cys Glu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
Leu Arg Ile Lys Gln Ile Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Asp Tyr
435 440 445
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Ser Gln
500 505 510
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu
515 520 525
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
Ile Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
Ser Leu Thr Gln Glu Glu Phe Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala
645 650 655
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu His Ala Ser Glu Lys
660 665 670
Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
Val Thr Arg Glu Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
Ile Glu Val Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Thr His Gln Tyr
740 745 750
Leu Gln Pro Ser Arg
755
<210> 71
<211> 4771
<212> DNA
<213> Artificial Sequence
<220>
<223> Vector genome CAG.CI.hMfn2.GA.link.miR1518.WPRE.SV40
<220>
<221> repeat_region
<222> (1)..(188)
<223> ITR
<220>
<221> misc_feature
<222> (192)..(1032)
<223> CAG (CBA)
<220>
<221> enhancer
<222> (194)..(436)
<223> CMV enhancer
<220>
<221> promoter
<222> (439)..(720)
<223> CB Promoter
<220>
<221> Intron
<222> (720)..(1127)
<223> Hybrid intron in CAG
<220>
<221> Intron
<222> (720)..(950)
<223> b-actin intron
<220>
<221> misc_feature
<222> (1158)..(1163)
<223> Kozak
<220>
<221> CDS
<222> (1164)..(3437)
<223> human Mfn2 optimized
<220>
<221> misc_feature
<222> (1379)..(1399)
<223> miR538 mut
<220>
<221> misc_feature
<222> (2534)..(2554)
<223> miR 1518 mutated
<220>
<221> misc_feature
<222> (3438)..(3519)
<223> linker p4271
<220>
<221> misc_feature
<222> (3520)..(3547)
<223> 5' flank
<220>
<221> misc_feature
<222> (3569)..(3587)
<223> loop
<220>
<221> misc_feature
<222> (3588)..(3606)
<223> rat miR 1518 sense
<220>
<221> misc_feature
<222> (3607)..(3651)
<223> 3' flank
<220>
<221> misc_feature
<222> (3678)..(4266)
<223> WRPE
<220>
<221> misc_feature
<222> (4355)..(4474)
<223> SV40 PA terminator
<220>
<221> repeat_region
<222> (4584)..(4771)
<223> ITR
<220>
<221> misc_feature
<222> (35488)..(3568)
<223> rat miR1518 AS
<400> 71
gctgcgcgct cgctcgctca ctgaggccgc ccgggcaaag cccgggcgtc gggcgacctt 60
tggtcgcccg gcctcagtga gcgagcgagc gcgcagagag ggagtggcca actccatcac 120
taggggttcc ttgtagttaa tgattaaccc gccatgctac ttatctacgt agccatgctc 180
taggaagagt accattgacg tcaataatga cgtatgttcc catagtaacg ccaataggga 240
ctttccattg acgtcaatgg gtggagtatt tacggtaaac tgcccacttg gcagtacatc 300
aagtgtatca tatgccaagt acgcccccta ttgacgtcaa tgacggtaaa tggcccgcct 360
ggcattatgc ccagtacatg accttatggg actttcctac ttggcagtac atctacgtat 420
tagtcatcgc tattaccatg gtcgaggtga gccccacgtt ctgcttcact ctccccatct 480
cccccccctc cccaccccca attttgtatt tatttatttt ttaattattt tgtgcagcga 540
tgggggcggg gggggggggg gggcgcgcgc caggcggggc ggggcggggc gaggggcggg 600
gcggggcgag gcggagaggt gcggcggcag ccaatcagag cggcgcgctc cgaaagtttc 660
cttttatggc gaggcggcgg cggcggcggc cctataaaaa gcgaagcgcg cggcgggcgg 720
gagtcgctgc gcgctgcctt cgccccgtgc cccgctccgc cgccgcctcg cgccgcccgc 780
cccggctctg actgaccgcg ttactcccac aggtgagcgg gcgggacggc ccttctcctc 840
cgggctgtaa ttagcgcttg gtttaatgac ggcttgtttc ttttctgtgg ctgcgtgaaa 900
gccttgaggg gctccgggag ggccctttgt gcggggggag cggctcgggg ctgtccgcgg 960
ggggacggct gccttcgggg gggacggggc agggcggggt tcggcttctg gcgtgtgacc 1020
ggcggctcta gagcctctgc taaccatgtt catgccttct tctttttcct acagctcctg 1080
ggcaacgtgc tggttattgt gctgtctcat cattttggca aagaattgga tcccgtacga 1140
cgcgtgctag caccggtgcc acc atg agc ctg ctg ttc agc cgg tgc aac agc 1193
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser
1 5 10
atc gtg acc gtg aag aaa aac aag cgg cac atg gcc gaa gtg aac gcc 1241
Ile Val Thr Val Lys Lys Asn Lys Arg His Met Ala Glu Val Asn Ala
15 20 25
tct cca ctg aag cac ttc gtg acc gcc aag aag aag atc aac ggc atc 1289
Ser Pro Leu Lys His Phe Val Thr Ala Lys Lys Lys Ile Asn Gly Ile
30 35 40
ttc gag cag ctg ggc gcc tac atc caa gag agc gcc acc ttc ctg gaa 1337
Phe Glu Gln Leu Gly Ala Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu
45 50 55
gat acc tac aga aac gcc gag ctg gac ccc gtg acc aca gag gaa cag 1385
Asp Thr Tyr Arg Asn Ala Glu Leu Asp Pro Val Thr Thr Glu Glu Gln
60 65 70
gtg ctg gat gtg aag ggc tac ctg agc aaa gtg cgg ggc atc tct gaa 1433
Val Leu Asp Val Lys Gly Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu
75 80 85 90
gtg ctg gcc aga cgg cat atg aag gtg gcc ttt ttc ggc cgg acc agc 1481
Val Leu Ala Arg Arg His Met Lys Val Ala Phe Phe Gly Arg Thr Ser
95 100 105
aac ggc aag agc acc gtg atc aat gcc atg ctg tgg gac aaa gtg ctg 1529
Asn Gly Lys Ser Thr Val Ile Asn Ala Met Leu Trp Asp Lys Val Leu
110 115 120
ccc tct gga atc ggc cac acc acc aac tgc ttt ctg aga gtg gaa ggc 1577
Pro Ser Gly Ile Gly His Thr Thr Asn Cys Phe Leu Arg Val Glu Gly
125 130 135
acc gac ggc cac gag gca ttt ctg ctg aca gag ggc tcc gag gaa aag 1625
Thr Asp Gly His Glu Ala Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys
140 145 150
cgg agc gcc aag aca gtg aac cag ctg gcc cat gct ctg cac cag gat 1673
Arg Ser Ala Lys Thr Val Asn Gln Leu Ala His Ala Leu His Gln Asp
155 160 165 170
aag cag ctg cat gcc gga agc ctg gtg tcc gtg atg tgg ccc aat agc 1721
Lys Gln Leu His Ala Gly Ser Leu Val Ser Val Met Trp Pro Asn Ser
175 180 185
aag tgc cct ctg ctg aag gac gac ctg gtg ctg atg gat agc ccc ggg 1769
Lys Cys Pro Leu Leu Lys Asp Asp Leu Val Leu Met Asp Ser Pro Gly
190 195 200
atc gat gtg acc acc gaa ctg gac agc tgg atc gac aag ttc tgc ctg 1817
Ile Asp Val Thr Thr Glu Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu
205 210 215
gac gcc gac gtg ttc gtg ctg gtg gcc aat agc gag agc acc ctg atg 1865
Asp Ala Asp Val Phe Val Leu Val Ala Asn Ser Glu Ser Thr Leu Met
220 225 230
cag acc gag aag cac ttt ttc cac aag gtg tcc gag cgg ctg agc aga 1913
Gln Thr Glu Lys His Phe Phe His Lys Val Ser Glu Arg Leu Ser Arg
235 240 245 250
ccc aat atc ttt atc ctg aac aac aga tgg gac gcc agc gcc agc gag 1961
Pro Asn Ile Phe Ile Leu Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu
255 260 265
ccc gag tat atg gaa gaa gtg cgg cgg cag cat atg gaa cgg tgc aca 2009
Pro Glu Tyr Met Glu Glu Val Arg Arg Gln His Met Glu Arg Cys Thr
270 275 280
tcc ttt ctg gtg gac gag ctg ggc gtc gtg gat aga tct cag gcc ggc 2057
Ser Phe Leu Val Asp Glu Leu Gly Val Val Asp Arg Ser Gln Ala Gly
285 290 295
gac aga atc ttc ttt gtg tcc gcc aaa gag gtg ctg aac gcc cgg att 2105
Asp Arg Ile Phe Phe Val Ser Ala Lys Glu Val Leu Asn Ala Arg Ile
300 305 310
cag aaa gcc cag gga atg cct gaa ggc gga ggt gca ctg gcc gag gga 2153
Gln Lys Ala Gln Gly Met Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly
315 320 325 330
ttt caa gtg cgg atg ttc gag ttc cag aac ttc gag cgg aga ttc gag 2201
Phe Gln Val Arg Met Phe Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu
335 340 345
gag tgc atc agc cag agc gcc gtc aag acc aag ttc gag cag cat acc 2249
Glu Cys Ile Ser Gln Ser Ala Val Lys Thr Lys Phe Glu Gln His Thr
350 355 360
gtg cgg gcc aag cag att gcc gaa gcc gtc aga ctg atc atg gac agc 2297
Val Arg Ala Lys Gln Ile Ala Glu Ala Val Arg Leu Ile Met Asp Ser
365 370 375
ctg cat atg gcc gcc aga gag cag cag gtc tac tgc gag gaa atg cgg 2345
Leu His Met Ala Ala Arg Glu Gln Gln Val Tyr Cys Glu Glu Met Arg
380 385 390
gaa gag aga cag gac cgg ctg aag ttc atc gac aag cag ctg gaa ctg 2393
Glu Glu Arg Gln Asp Arg Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu
395 400 405 410
ctg gcc cag gac tac aag ctg cgg atc aag cag atc acc gaa gag gtg 2441
Leu Ala Gln Asp Tyr Lys Leu Arg Ile Lys Gln Ile Thr Glu Glu Val
415 420 425
gaa aga cag gtg tcc acc gct atg gcc gag gaa atc aga cgg ctg agc 2489
Glu Arg Gln Val Ser Thr Ala Met Ala Glu Glu Ile Arg Arg Leu Ser
430 435 440
gtg ctg gtc gac gac tac cag atg gac ttt cac ccc tct cca gtg gtg 2537
Val Leu Val Asp Asp Tyr Gln Met Asp Phe His Pro Ser Pro Val Val
445 450 455
ctg aaa gtc tac aaa aac gag ctg cac cgg cac atc gag gaa ggc ctg 2585
Leu Lys Val Tyr Lys Asn Glu Leu His Arg His Ile Glu Glu Gly Leu
460 465 470
ggc aga aac atg agc gac aga tgc agc acc gcc atc acc aat agc ctg 2633
Gly Arg Asn Met Ser Asp Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu
475 480 485 490
cag acc atg cag cag gac atg atc gac ggc ctg aaa cct ctg ctg cct 2681
Gln Thr Met Gln Gln Asp Met Ile Asp Gly Leu Lys Pro Leu Leu Pro
495 500 505
gtg tcc gtc aga tcc cag atc gat atg ctg gtg ccc cgg cag tgc ttt 2729
Val Ser Val Arg Ser Gln Ile Asp Met Leu Val Pro Arg Gln Cys Phe
510 515 520
agc ctg aac tac gac ctg aac tgc gac aag ctg tgc gcc gat ttc caa 2777
Ser Leu Asn Tyr Asp Leu Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln
525 530 535
gag gac atc gag ttt cac ttc agc ctc ggc tgg aca atg ctg gtc aac 2825
Glu Asp Ile Glu Phe His Phe Ser Leu Gly Trp Thr Met Leu Val Asn
540 545 550
aga ttt ctg ggc ccc aag aac agc aga cgg gcc ctg atg ggc tac aac 2873
Arg Phe Leu Gly Pro Lys Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn
555 560 565 570
gat cag gtg cag agg ccc att cct ctg aca ccc gcc aat cct agc atg 2921
Asp Gln Val Gln Arg Pro Ile Pro Leu Thr Pro Ala Asn Pro Ser Met
575 580 585
cct cca ctg cct cag ggc agc ctg aca caa gag gaa ttc atg gtg tct 2969
Pro Pro Leu Pro Gln Gly Ser Leu Thr Gln Glu Glu Phe Met Val Ser
590 595 600
atg gtc acc ggc ctg gcc agc ctg acc agc aga aca tct atg ggc atc 3017
Met Val Thr Gly Leu Ala Ser Leu Thr Ser Arg Thr Ser Met Gly Ile
605 610 615
ctg gtc gtc ggc ggc gtt gtg tgg aaa gct gtt ggc tgg cgg ctg atc 3065
Leu Val Val Gly Gly Val Val Trp Lys Ala Val Gly Trp Arg Leu Ile
620 625 630
gcc ctg agc ttt ggc ctg tat ggc ctg ctg tac gtg tac gag aga ctg 3113
Ala Leu Ser Phe Gly Leu Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu
635 640 645 650
acc tgg acc acc aag gcc aaa gag cgg gcc ttc aag cgg cag ttt gtg 3161
Thr Trp Thr Thr Lys Ala Lys Glu Arg Ala Phe Lys Arg Gln Phe Val
655 660 665
gaa cac gcc tcc gag aaa ctg cag ctg gtg atc agc tac acc ggc agc 3209
Glu His Ala Ser Glu Lys Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser
670 675 680
aat tgc agc cac cag gtg cag caa gag ctg tcc gga aca ttc gcc cac 3257
Asn Cys Ser His Gln Val Gln Gln Glu Leu Ser Gly Thr Phe Ala His
685 690 695
ctg tgt cag cag gtc gac gtg acc aga gag aac ctg gaa caa gag atc 3305
Leu Cys Gln Gln Val Asp Val Thr Arg Glu Asn Leu Glu Gln Glu Ile
700 705 710
gcc gcc atg aat aag aaa atc gag gtg ctc gac tcc ctg cag agc aag 3353
Ala Ala Met Asn Lys Lys Ile Glu Val Leu Asp Ser Leu Gln Ser Lys
715 720 725 730
gcc aag ctg ctg aga aac aag gcc ggc tgg ctg gac agc gag ctg aat 3401
Ala Lys Leu Leu Arg Asn Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn
735 740 745
atg ttc acc cac cag tac ctg cag cct agc cgc taa taaagcggcc 3447
Met Phe Thr His Gln Tyr Leu Gln Pro Ser Arg
750 755
gcaagcttgc acccgtacct ttgggagcgc gcgccctcgt cgtgtcgtga cgtcacccgt 3507
tctgttggat ccctggaggc ttgctgaagg ctgtatgctg ttcttataaa ccttgaggac 3567
agttttggcc actgactgac tgtcctcagt ttataagaac aggacacaag gcctgttact 3627
agcactcaca tggaacaaat ggcccagatc ttaagcttct cgagatcgat aatcaacctc 3687
tggattacaa aatttgtgaa agattgactg gtattcttaa ctatgttgct ccttttacgc 3747
tatgtggata cgctgcttta atgcctttgt atcatgctat tgcttcccgt atggctttca 3807
ttttctcctc cttgtataaa tcctggttgc tgtctcttta tgaggagttg tggcccgttg 3867
tcaggcaacg tggcgtggtg tgcactgtgt ttgctgacgc aacccccact ggttggggca 3927
ttgccaccac ctgtcagctc ctttccggga ctttcgcttt ccccctccct attgccacgg 3987
cggaactcat cgccgcctgc cttgcccgct gctggacagg ggctcggctg ttgggcactg 4047
acaattccgt ggtgttgtcg gggaaatcat cgtcctttcc ttggctgctc gcctgtgttg 4107
ccacctggat tctgcgcggg acgcccttct gctacgtccc ttcggccctc aatccagcgg 4167
accttccttc ccgcggcctg ctgccggctc tgcggcctct tccgcgtctt cgccttcgcc 4227
ctcagacgag tcggatctcc ctttgggccg cctccccgcc tgctgatcgc cctgagcctg 4287
gccctggtga ccaacagcca ggtgcaattg ctagagtcga ctctagagcg gccgcttcga 4347
gcagacatga taagatacat tgatgagttt ggacaaacca caactagaat gcagtgaaaa 4407
aaatgcttta tttgtgaaat ttgtgatgct attgctttat ttgtaaccat tataagctgc 4467
aataaacaag ttaacaacaa caattgcatt cattttatgt ttcaggttca gggggagatg 4527
tgggaggttt tttaaagcaa gtaaaacctc tacaaatgtg gtaaaatcga taaggatctt 4587
cctagagcat ggctacgtag ataagtagca tggcgggtta atcattaact acaaggaacc 4647
cctagtgatg gagttggcca ctccctctct gcgcgctcgc tcgctcactg aggccgggcg 4707
accaaaggtc gcccgacgcc cgggctttgc ccgggcggcc tcagtgagcg agcgagcgcg 4767
cagc 4771
<210> 72
<211> 757
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 72
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
Asn Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala
50 55 60
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
Thr Thr Asn Cys Phe Leu Arg Val Glu Gly Thr Asp Gly His Glu Ala
130 135 140
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Arg Ser Ala Lys Thr Val
145 150 155 160
Asn Gln Leu Ala His Ala Leu His Gln Asp Lys Gln Leu His Ala Gly
165 170 175
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys His Phe
225 230 235 240
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
Leu Gly Val Val Asp Arg Ser Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
Ser Ala Lys Glu Val Leu Asn Ala Arg Ile Gln Lys Ala Gln Gly Met
305 310 315 320
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Met Ala Ala Arg
370 375 380
Glu Gln Gln Val Tyr Cys Glu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
Leu Arg Ile Lys Gln Ile Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Asp Tyr
435 440 445
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Ser Gln
500 505 510
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu
515 520 525
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
Ile Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
Ser Leu Thr Gln Glu Glu Phe Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala
645 650 655
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu His Ala Ser Glu Lys
660 665 670
Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
Val Thr Arg Glu Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
Ile Glu Val Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Thr His Gln Tyr
740 745 750
Leu Gln Pro Ser Arg
755
<210> 73
<211> 4559
<212> DNA
<213> Artificial Sequence
<220>
<223> Vector genome CAG.CI.hMfn2.GA.WPRE.SV40
<220>
<221> repeat_region
<222> (1)..(188)
<223> ITR
<220>
<221> misc_feature
<222> (192)..(1032)
<223> CAG (CBA)
<220>
<221> enhancer
<222> (194)..(1032)
<223> CMV enhancer
<220>
<221> promoter
<222> (439)..(720)
<223> CB promoter
<220>
<221> Intron
<222> (720)..(1127)
<223> Hybrid intron in CAG
<220>
<221> Intron
<222> (720)..(950)
<223> b-actin intron
<220>
<221> misc_feature
<222> (1158)..(1163)
<223> Kozak
<220>
<221> CDS
<222> (1164)..(3437)
<223> huamn Mfn2 engineered
<220>
<221> misc_feature
<222> (1379)..(1399)
<223> miR538 mut
<220>
<221> misc_feature
<222> (2534)..(2554)
<223> miR1518 mutated
<220>
<221> misc_feature
<222> (3466)..(4054)
<223> WRPE
<220>
<221> misc_feature
<222> (4143)..(4262)
<223> SV 40 PA temrinator
<220>
<221> rep_origin
<222> (4372)..(4559)
<223> ITR
<400> 73
gctgcgcgct cgctcgctca ctgaggccgc ccgggcaaag cccgggcgtc gggcgacctt 60
tggtcgcccg gcctcagtga gcgagcgagc gcgcagagag ggagtggcca actccatcac 120
taggggttcc ttgtagttaa tgattaaccc gccatgctac ttatctacgt agccatgctc 180
taggaagagt accattgacg tcaataatga cgtatgttcc catagtaacg ccaataggga 240
ctttccattg acgtcaatgg gtggagtatt tacggtaaac tgcccacttg gcagtacatc 300
aagtgtatca tatgccaagt acgcccccta ttgacgtcaa tgacggtaaa tggcccgcct 360
ggcattatgc ccagtacatg accttatggg actttcctac ttggcagtac atctacgtat 420
tagtcatcgc tattaccatg gtcgaggtga gccccacgtt ctgcttcact ctccccatct 480
cccccccctc cccaccccca attttgtatt tatttatttt ttaattattt tgtgcagcga 540
tgggggcggg gggggggggg gggcgcgcgc caggcggggc ggggcggggc gaggggcggg 600
gcggggcgag gcggagaggt gcggcggcag ccaatcagag cggcgcgctc cgaaagtttc 660
cttttatggc gaggcggcgg cggcggcggc cctataaaaa gcgaagcgcg cggcgggcgg 720
gagtcgctgc gcgctgcctt cgccccgtgc cccgctccgc cgccgcctcg cgccgcccgc 780
cccggctctg actgaccgcg ttactcccac aggtgagcgg gcgggacggc ccttctcctc 840
cgggctgtaa ttagcgcttg gtttaatgac ggcttgtttc ttttctgtgg ctgcgtgaaa 900
gccttgaggg gctccgggag ggccctttgt gcggggggag cggctcgggg ctgtccgcgg 960
ggggacggct gccttcgggg gggacggggc agggcggggt tcggcttctg gcgtgtgacc 1020
ggcggctcta gagcctctgc taaccatgtt catgccttct tctttttcct acagctcctg 1080
ggcaacgtgc tggttattgt gctgtctcat cattttggca aagaattgga tcccgtacga 1140
cgcgtgctag caccggtgcc acc atg agc ctg ctg ttc agc cgg tgc aac agc 1193
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser
1 5 10
atc gtg acc gtg aag aaa aac aag cgg cac atg gcc gaa gtg aac gcc 1241
Ile Val Thr Val Lys Lys Asn Lys Arg His Met Ala Glu Val Asn Ala
15 20 25
tct cca ctg aag cac ttc gtg acc gcc aag aag aag atc aac ggc atc 1289
Ser Pro Leu Lys His Phe Val Thr Ala Lys Lys Lys Ile Asn Gly Ile
30 35 40
ttc gag cag ctg ggc gcc tac atc caa gag agc gcc acc ttc ctg gaa 1337
Phe Glu Gln Leu Gly Ala Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu
45 50 55
gat acc tac aga aac gcc gag ctg gac ccc gtg acc aca gag gaa cag 1385
Asp Thr Tyr Arg Asn Ala Glu Leu Asp Pro Val Thr Thr Glu Glu Gln
60 65 70
gtg ctg gat gtg aag ggc tac ctg agc aaa gtg cgg ggc atc tct gaa 1433
Val Leu Asp Val Lys Gly Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu
75 80 85 90
gtg ctg gcc aga cgg cat atg aag gtg gcc ttt ttc ggc cgg acc agc 1481
Val Leu Ala Arg Arg His Met Lys Val Ala Phe Phe Gly Arg Thr Ser
95 100 105
aac ggc aag agc acc gtg atc aat gcc atg ctg tgg gac aaa gtg ctg 1529
Asn Gly Lys Ser Thr Val Ile Asn Ala Met Leu Trp Asp Lys Val Leu
110 115 120
ccc tct gga atc ggc cac acc acc aac tgc ttt ctg aga gtg gaa ggc 1577
Pro Ser Gly Ile Gly His Thr Thr Asn Cys Phe Leu Arg Val Glu Gly
125 130 135
acc gac ggc cac gag gca ttt ctg ctg aca gag ggc tcc gag gaa aag 1625
Thr Asp Gly His Glu Ala Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys
140 145 150
cgg agc gcc aag aca gtg aac cag ctg gcc cat gct ctg cac cag gat 1673
Arg Ser Ala Lys Thr Val Asn Gln Leu Ala His Ala Leu His Gln Asp
155 160 165 170
aag cag ctg cat gcc gga agc ctg gtg tcc gtg atg tgg ccc aat agc 1721
Lys Gln Leu His Ala Gly Ser Leu Val Ser Val Met Trp Pro Asn Ser
175 180 185
aag tgc cct ctg ctg aag gac gac ctg gtg ctg atg gat agc ccc ggg 1769
Lys Cys Pro Leu Leu Lys Asp Asp Leu Val Leu Met Asp Ser Pro Gly
190 195 200
atc gat gtg acc acc gaa ctg gac agc tgg atc gac aag ttc tgc ctg 1817
Ile Asp Val Thr Thr Glu Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu
205 210 215
gac gcc gac gtg ttc gtg ctg gtg gcc aat agc gag agc acc ctg atg 1865
Asp Ala Asp Val Phe Val Leu Val Ala Asn Ser Glu Ser Thr Leu Met
220 225 230
cag acc gag aag cac ttt ttc cac aag gtg tcc gag cgg ctg agc aga 1913
Gln Thr Glu Lys His Phe Phe His Lys Val Ser Glu Arg Leu Ser Arg
235 240 245 250
ccc aat atc ttt atc ctg aac aac aga tgg gac gcc agc gcc agc gag 1961
Pro Asn Ile Phe Ile Leu Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu
255 260 265
ccc gag tat atg gaa gaa gtg cgg cgg cag cat atg gaa cgg tgc aca 2009
Pro Glu Tyr Met Glu Glu Val Arg Arg Gln His Met Glu Arg Cys Thr
270 275 280
tcc ttt ctg gtg gac gag ctg ggc gtc gtg gat aga tct cag gcc ggc 2057
Ser Phe Leu Val Asp Glu Leu Gly Val Val Asp Arg Ser Gln Ala Gly
285 290 295
gac aga atc ttc ttt gtg tcc gcc aaa gag gtg ctg aac gcc cgg att 2105
Asp Arg Ile Phe Phe Val Ser Ala Lys Glu Val Leu Asn Ala Arg Ile
300 305 310
cag aaa gcc cag gga atg cct gaa ggc gga ggt gca ctg gcc gag gga 2153
Gln Lys Ala Gln Gly Met Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly
315 320 325 330
ttt caa gtg cgg atg ttc gag ttc cag aac ttc gag cgg aga ttc gag 2201
Phe Gln Val Arg Met Phe Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu
335 340 345
gag tgc atc agc cag agc gcc gtc aag acc aag ttc gag cag cat acc 2249
Glu Cys Ile Ser Gln Ser Ala Val Lys Thr Lys Phe Glu Gln His Thr
350 355 360
gtg cgg gcc aag cag att gcc gaa gcc gtc aga ctg atc atg gac agc 2297
Val Arg Ala Lys Gln Ile Ala Glu Ala Val Arg Leu Ile Met Asp Ser
365 370 375
ctg cat atg gcc gcc aga gag cag cag gtc tac tgc gag gaa atg cgg 2345
Leu His Met Ala Ala Arg Glu Gln Gln Val Tyr Cys Glu Glu Met Arg
380 385 390
gaa gag aga cag gac cgg ctg aag ttc atc gac aag cag ctg gaa ctg 2393
Glu Glu Arg Gln Asp Arg Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu
395 400 405 410
ctg gcc cag gac tac aag ctg cgg atc aag cag atc acc gaa gag gtg 2441
Leu Ala Gln Asp Tyr Lys Leu Arg Ile Lys Gln Ile Thr Glu Glu Val
415 420 425
gaa aga cag gtg tcc acc gct atg gcc gag gaa atc aga cgg ctg agc 2489
Glu Arg Gln Val Ser Thr Ala Met Ala Glu Glu Ile Arg Arg Leu Ser
430 435 440
gtg ctg gtc gac gac tac cag atg gac ttt cac ccc tct cca gtg gtg 2537
Val Leu Val Asp Asp Tyr Gln Met Asp Phe His Pro Ser Pro Val Val
445 450 455
ctg aaa gtc tac aaa aac gag ctg cac cgg cac atc gag gaa ggc ctg 2585
Leu Lys Val Tyr Lys Asn Glu Leu His Arg His Ile Glu Glu Gly Leu
460 465 470
ggc aga aac atg agc gac aga tgc agc acc gcc atc acc aat agc ctg 2633
Gly Arg Asn Met Ser Asp Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu
475 480 485 490
cag acc atg cag cag gac atg atc gac ggc ctg aaa cct ctg ctg cct 2681
Gln Thr Met Gln Gln Asp Met Ile Asp Gly Leu Lys Pro Leu Leu Pro
495 500 505
gtg tcc gtc aga tcc cag atc gat atg ctg gtg ccc cgg cag tgc ttt 2729
Val Ser Val Arg Ser Gln Ile Asp Met Leu Val Pro Arg Gln Cys Phe
510 515 520
agc ctg aac tac gac ctg aac tgc gac aag ctg tgc gcc gat ttc caa 2777
Ser Leu Asn Tyr Asp Leu Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln
525 530 535
gag gac atc gag ttt cac ttc agc ctc ggc tgg aca atg ctg gtc aac 2825
Glu Asp Ile Glu Phe His Phe Ser Leu Gly Trp Thr Met Leu Val Asn
540 545 550
aga ttt ctg ggc ccc aag aac agc aga cgg gcc ctg atg ggc tac aac 2873
Arg Phe Leu Gly Pro Lys Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn
555 560 565 570
gat cag gtg cag agg ccc att cct ctg aca ccc gcc aat cct agc atg 2921
Asp Gln Val Gln Arg Pro Ile Pro Leu Thr Pro Ala Asn Pro Ser Met
575 580 585
cct cca ctg cct cag ggc agc ctg aca caa gag gaa ttc atg gtg tct 2969
Pro Pro Leu Pro Gln Gly Ser Leu Thr Gln Glu Glu Phe Met Val Ser
590 595 600
atg gtc acc ggc ctg gcc agc ctg acc agc aga aca tct atg ggc atc 3017
Met Val Thr Gly Leu Ala Ser Leu Thr Ser Arg Thr Ser Met Gly Ile
605 610 615
ctg gtc gtc ggc ggc gtt gtg tgg aaa gct gtt ggc tgg cgg ctg atc 3065
Leu Val Val Gly Gly Val Val Trp Lys Ala Val Gly Trp Arg Leu Ile
620 625 630
gcc ctg agc ttt ggc ctg tat ggc ctg ctg tac gtg tac gag aga ctg 3113
Ala Leu Ser Phe Gly Leu Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu
635 640 645 650
acc tgg acc acc aag gcc aaa gag cgg gcc ttc aag cgg cag ttt gtg 3161
Thr Trp Thr Thr Lys Ala Lys Glu Arg Ala Phe Lys Arg Gln Phe Val
655 660 665
gaa cac gcc tcc gag aaa ctg cag ctg gtg atc agc tac acc ggc agc 3209
Glu His Ala Ser Glu Lys Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser
670 675 680
aat tgc agc cac cag gtg cag caa gag ctg tcc gga aca ttc gcc cac 3257
Asn Cys Ser His Gln Val Gln Gln Glu Leu Ser Gly Thr Phe Ala His
685 690 695
ctg tgt cag cag gtc gac gtg acc aga gag aac ctg gaa caa gag atc 3305
Leu Cys Gln Gln Val Asp Val Thr Arg Glu Asn Leu Glu Gln Glu Ile
700 705 710
gcc gcc atg aat aag aaa atc gag gtg ctc gac tcc ctg cag agc aag 3353
Ala Ala Met Asn Lys Lys Ile Glu Val Leu Asp Ser Leu Gln Ser Lys
715 720 725 730
gcc aag ctg ctg aga aac aag gcc ggc tgg ctg gac agc gag ctg aat 3401
Ala Lys Leu Leu Arg Asn Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn
735 740 745
atg ttc acc cac cag tac ctg cag cct agc cgc taa taatgtactt 3447
Met Phe Thr His Gln Tyr Leu Gln Pro Ser Arg
750 755
aagcttctcg agatcgataa tcaacctctg gattacaaaa tttgtgaaag attgactggt 3507
attcttaact atgttgctcc ttttacgcta tgtggatacg ctgctttaat gcctttgtat 3567
catgctattg cttcccgtat ggctttcatt ttctcctcct tgtataaatc ctggttgctg 3627
tctctttatg aggagttgtg gcccgttgtc aggcaacgtg gcgtggtgtg cactgtgttt 3687
gctgacgcaa cccccactgg ttggggcatt gccaccacct gtcagctcct ttccgggact 3747
ttcgctttcc ccctccctat tgccacggcg gaactcatcg ccgcctgcct tgcccgctgc 3807
tggacagggg ctcggctgtt gggcactgac aattccgtgg tgttgtcggg gaaatcatcg 3867
tcctttcctt ggctgctcgc ctgtgttgcc acctggattc tgcgcgggac gcccttctgc 3927
tacgtccctt cggccctcaa tccagcggac cttccttccc gcggcctgct gccggctctg 3987
cggcctcttc cgcgtcttcg ccttcgccct cagacgagtc ggatctccct ttgggccgcc 4047
tccccgcctg ctgatcgccc tgagcctggc cctggtgacc aacagccagg tgcaattgct 4107
agagtcgact ctagagcggc cgcttcgagc agacatgata agatacattg atgagtttgg 4167
acaaaccaca actagaatgc agtgaaaaaa atgctttatt tgtgaaattt gtgatgctat 4227
tgctttattt gtaaccatta taagctgcaa taaacaagtt aacaacaaca attgcattca 4287
ttttatgttt caggttcagg gggagatgtg ggaggttttt taaagcaagt aaaacctcta 4347
caaatgtggt aaaatcgata aggatcttcc tagagcatgg ctacgtagat aagtagcatg 4407
gcgggttaat cattaactac aaggaacccc tagtgatgga gttggccact ccctctctgc 4467
gcgctcgctc gctcactgag gccgggcgac caaaggtcgc ccgacgcccg ggctttgccc 4527
gggcggcctc agtgagcgag cgagcgcgca gc 4559
<210> 74
<211> 757
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 74
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
Asn Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala
50 55 60
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
Thr Thr Asn Cys Phe Leu Arg Val Glu Gly Thr Asp Gly His Glu Ala
130 135 140
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Arg Ser Ala Lys Thr Val
145 150 155 160
Asn Gln Leu Ala His Ala Leu His Gln Asp Lys Gln Leu His Ala Gly
165 170 175
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys His Phe
225 230 235 240
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
Leu Gly Val Val Asp Arg Ser Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
Ser Ala Lys Glu Val Leu Asn Ala Arg Ile Gln Lys Ala Gln Gly Met
305 310 315 320
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Met Ala Ala Arg
370 375 380
Glu Gln Gln Val Tyr Cys Glu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
Leu Arg Ile Lys Gln Ile Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Asp Tyr
435 440 445
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Ser Gln
500 505 510
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu
515 520 525
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
Ile Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
Ser Leu Thr Gln Glu Glu Phe Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala
645 650 655
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu His Ala Ser Glu Lys
660 665 670
Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
Val Thr Arg Glu Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
Ile Glu Val Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Thr His Gln Tyr
740 745 750
Leu Gln Pro Ser Arg
755
<210> 75
<211> 4821
<212> DNA
<213> Artificial Sequence
<220>
<223> Vector genome CB7.CI.hMfn2.GA.link.miR538.rBG
<220>
<221> repeat_region
<222> (1)..(130)
<223> ITR
<220>
<221> enhancer
<222> (259)..(562)
<223> CMV enhancer
<220>
<221> promoter
<222> (561)..(842)
<223> CB7 promoter
<220>
<221> Intron
<222> (935)..(1907)
<223> chicken beta-actin intron
<220>
<221> misc_feature
<222> (1953)..(1958)
<223> Kozak
<220>
<221> CDS
<222> (1959)..(4232)
<223> human Mfn2 engineered
<220>
<221> misc_feature
<222> (2174)..(2194)
<223> miR538 mut
<220>
<221> misc_feature
<222> (3329)..(3349)
<223> miR1518
<220>
<221> misc_feature
<222> (4233)..(4314)
<223> linker p5271
<220>
<221> misc_feature
<222> (4315)..(4342)
<223> 5' flank
<220>
<221> misc_feature
<222> (4343)..(4363)
<223> miR538 AS
<220>
<221> misc_feature
<222> (4364)..(4382)
<223> loop
<220>
<221> misc_feature
<222> (4383)..(4401)
<223> miR538 Sense
<220>
<221> misc_feature
<222> (4402)..(4446)
<223> 3' flank
<220>
<221> polyA_signal
<222> (4500)..(4626)
<223> rabbit globin poly A
<220>
<221> repeat_region
<222> (4692)..(4821)
<223> ITR
<400> 75
ctgcgcgctc gctcgctcac tgaggccgcc cgggcaaagc ccgggcgtcg ggcgaccttt 60
ggtcgcccgg cctcagtgag cgagcgagcg cgcagagagg gagtggccaa ctccatcact 120
aggggttcct tgtagttaat gattaacccg ccatgctact tatctacgta gccatgctct 180
aggaagatct gatatcacta gttattaata gtaatcaatt acggggtcat tagttcatag 240
cccatatatg gagttccgcg ttacataact tacggtaaat ggcccgcctg gctgaccgcc 300
caacgacccc cgcccattga cgtcaataat gacgtatgtt cccatagtaa cgccaatagg 360
gactttccat tgacgtcaat gggtggagta tttacggtaa actgcccact tggcagtaca 420
tcaagtgtat catatgccaa gtacgccccc tattgacgtc aatgacggta aatggcccgc 480
ctggcattat gcccagtaca tgaccttatg ggactttcct acttggcagt acatctacgt 540
attagtcatc gctattacca tggtcgaggt gagccccacg ttctgcttca ctctccccat 600
ctcccccccc tccccacccc caattttgta tttatttatt ttttaattat tttgtgcagc 660
gatgggggcg gggggggggg gggggcgcgc gccaggcggg gcggggcggg gcgaggggcg 720
gggcggggcg aggcggagag gtgcggcggc agccaatcag agcggcgcgc tccgaaagtt 780
tccttttatg gcgaggcggc ggcggcggcg gccctataaa aagcgaagcg cgcggcgggc 840
gggagtcgct gcgcgctgcc ttcgccccgt gccccgctcc gccgccgcct cgcgccgccc 900
gccccggctc tgactgaccg cgttactccc acaggtgagc gggcgggacg gcccttctcc 960
tccgggctgt aattagcgct tggtttaatg acggcttgtt tcttttctgt ggctgcgtga 1020
aagccttgag gggctccggg agggcccttt gtgcgggggg agcggctcgg ggggtgcgtg 1080
cgtgtgtgtg tgcgtgggga gcgccgcgtg cggctccgcg ctgcccggcg gctgtgagcg 1140
ctgcgggcgc ggcgcggggc tttgtgcgct ccgcagtgtg cgcgagggga gcgcggccgg 1200
gggcggtgcc ccgcggtgcg gggggggctg cgaggggaac aaaggctgcg tgcggggtgt 1260
gtgcgtgggg gggtgagcag ggggtgtggg cgcgtcggtc gggctgcaac cccccctgca 1320
cccccctccc cgagttgctg agcacggccc ggcttcgggt gcggggctcc gtacggggcg 1380
tggcgcgggg ctcgccgtgc cgggcggggg gtggcggcag gtgggggtgc cgggcggggc 1440
ggggccgcct cgggccgggg agggctcggg ggaggggcgc ggcggccccc ggagcgccgg 1500
cggctgtcga ggcgcggcga gccgcagcca ttgcctttta tggtaatcgt gcgagagggc 1560
gcagggactt cctttgtccc aaatctgtgc ggagccgaaa tctgggaggc gccgccgcac 1620
cccctctagc gggcgcgggg cgaagcggtg cggcgccggc aggaaggaaa tgggcgggga 1680
gggccttcgt gcgtcgccgc gccgccgtcc ccttctccct ctccagcctc ggggctgtcc 1740
gcggggggac ggctgccttc gggggggacg gggcagggcg gggttcggct tctggcgtgt 1800
gaccggcggc tctagagcct ctgctaacca tgttcatgcc ttcttctttt tcctacagct 1860
cctgggcaac gtgctggtta ttgtgctgtc tcatcatttt ggcaaagaat tcacgcgtgc 1920
taggatcccg tacgacgcgt gctagcaccg gtgccacc atg agc ctg ctg ttc agc 1976
Met Ser Leu Leu Phe Ser
1 5
cgg tgc aac agc atc gtg acc gtg aag aaa aac aag cgg cac atg gcc 2024
Arg Cys Asn Ser Ile Val Thr Val Lys Lys Asn Lys Arg His Met Ala
10 15 20
gaa gtg aac gcc tct cca ctg aag cac ttc gtg acc gcc aag aag aag 2072
Glu Val Asn Ala Ser Pro Leu Lys His Phe Val Thr Ala Lys Lys Lys
25 30 35
atc aac ggc atc ttc gag cag ctg ggc gcc tac atc caa gag agc gcc 2120
Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala Tyr Ile Gln Glu Ser Ala
40 45 50
acc ttc ctg gaa gat acc tac aga aac gcc gag ctg gac ccc gtg acc 2168
Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala Glu Leu Asp Pro Val Thr
55 60 65 70
aca gag gaa cag gtg ctg gat gtg aag ggc tac ctg agc aaa gtg cgg 2216
Thr Glu Glu Gln Val Leu Asp Val Lys Gly Tyr Leu Ser Lys Val Arg
75 80 85
ggc atc tct gaa gtg ctg gcc aga cgg cat atg aag gtg gcc ttt ttc 2264
Gly Ile Ser Glu Val Leu Ala Arg Arg His Met Lys Val Ala Phe Phe
90 95 100
ggc cgg acc agc aac ggc aag agc acc gtg atc aat gcc atg ctg tgg 2312
Gly Arg Thr Ser Asn Gly Lys Ser Thr Val Ile Asn Ala Met Leu Trp
105 110 115
gac aaa gtg ctg ccc tct gga atc ggc cac acc acc aac tgc ttt ctg 2360
Asp Lys Val Leu Pro Ser Gly Ile Gly His Thr Thr Asn Cys Phe Leu
120 125 130
aga gtg gaa ggc acc gac ggc cac gag gca ttt ctg ctg aca gag ggc 2408
Arg Val Glu Gly Thr Asp Gly His Glu Ala Phe Leu Leu Thr Glu Gly
135 140 145 150
tcc gag gaa aag cgg agc gcc aag aca gtg aac cag ctg gcc cat gct 2456
Ser Glu Glu Lys Arg Ser Ala Lys Thr Val Asn Gln Leu Ala His Ala
155 160 165
ctg cac cag gat aag cag ctg cat gcc gga agc ctg gtg tcc gtg atg 2504
Leu His Gln Asp Lys Gln Leu His Ala Gly Ser Leu Val Ser Val Met
170 175 180
tgg ccc aat agc aag tgc cct ctg ctg aag gac gac ctg gtg ctg atg 2552
Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys Asp Asp Leu Val Leu Met
185 190 195
gat agc ccc ggg atc gat gtg acc acc gaa ctg gac agc tgg atc gac 2600
Asp Ser Pro Gly Ile Asp Val Thr Thr Glu Leu Asp Ser Trp Ile Asp
200 205 210
aag ttc tgc ctg gac gcc gac gtg ttc gtg ctg gtg gcc aat agc gag 2648
Lys Phe Cys Leu Asp Ala Asp Val Phe Val Leu Val Ala Asn Ser Glu
215 220 225 230
agc acc ctg atg cag acc gag aag cac ttt ttc cac aag gtg tcc gag 2696
Ser Thr Leu Met Gln Thr Glu Lys His Phe Phe His Lys Val Ser Glu
235 240 245
cgg ctg agc aga ccc aat atc ttt atc ctg aac aac aga tgg gac gcc 2744
Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu Asn Asn Arg Trp Asp Ala
250 255 260
agc gcc agc gag ccc gag tat atg gaa gaa gtg cgg cgg cag cat atg 2792
Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu Val Arg Arg Gln His Met
265 270 275
gaa cgg tgc aca tcc ttt ctg gtg gac gag ctg ggc gtc gtg gat aga 2840
Glu Arg Cys Thr Ser Phe Leu Val Asp Glu Leu Gly Val Val Asp Arg
280 285 290
tct cag gcc ggc gac aga atc ttc ttt gtg tcc gcc aaa gag gtg ctg 2888
Ser Gln Ala Gly Asp Arg Ile Phe Phe Val Ser Ala Lys Glu Val Leu
295 300 305 310
aac gcc cgg att cag aaa gcc cag gga atg cct gaa ggc gga ggt gca 2936
Asn Ala Arg Ile Gln Lys Ala Gln Gly Met Pro Glu Gly Gly Gly Ala
315 320 325
ctg gcc gag gga ttt caa gtg cgg atg ttc gag ttc cag aac ttc gag 2984
Leu Ala Glu Gly Phe Gln Val Arg Met Phe Glu Phe Gln Asn Phe Glu
330 335 340
cgg aga ttc gag gag tgc atc agc cag agc gcc gtc aag acc aag ttc 3032
Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser Ala Val Lys Thr Lys Phe
345 350 355
gag cag cat acc gtg cgg gcc aag cag att gcc gaa gcc gtc aga ctg 3080
Glu Gln His Thr Val Arg Ala Lys Gln Ile Ala Glu Ala Val Arg Leu
360 365 370
atc atg gac agc ctg cat atg gcc gcc aga gag cag cag gtc tac tgc 3128
Ile Met Asp Ser Leu His Met Ala Ala Arg Glu Gln Gln Val Tyr Cys
375 380 385 390
gag gaa atg cgg gaa gag aga cag gac cgg ctg aag ttc atc gac aag 3176
Glu Glu Met Arg Glu Glu Arg Gln Asp Arg Leu Lys Phe Ile Asp Lys
395 400 405
cag ctg gaa ctg ctg gcc cag gac tac aag ctg cgg atc aag cag atc 3224
Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys Leu Arg Ile Lys Gln Ile
410 415 420
acc gaa gag gtg gaa aga cag gtg tcc acc gct atg gcc gag gaa atc 3272
Thr Glu Glu Val Glu Arg Gln Val Ser Thr Ala Met Ala Glu Glu Ile
425 430 435
aga cgg ctg agc gtg ctg gtc gac gac tac cag atg gac ttt cac ccc 3320
Arg Arg Leu Ser Val Leu Val Asp Asp Tyr Gln Met Asp Phe His Pro
440 445 450
tct cca gtg gtg ctg aaa gtc tac aaa aac gag ctg cac cgg cac atc 3368
Ser Pro Val Val Leu Lys Val Tyr Lys Asn Glu Leu His Arg His Ile
455 460 465 470
gag gaa ggc ctg ggc aga aac atg agc gac aga tgc agc acc gcc atc 3416
Glu Glu Gly Leu Gly Arg Asn Met Ser Asp Arg Cys Ser Thr Ala Ile
475 480 485
acc aat agc ctg cag acc atg cag cag gac atg atc gac ggc ctg aaa 3464
Thr Asn Ser Leu Gln Thr Met Gln Gln Asp Met Ile Asp Gly Leu Lys
490 495 500
cct ctg ctg cct gtg tcc gtc aga tcc cag atc gat atg ctg gtg ccc 3512
Pro Leu Leu Pro Val Ser Val Arg Ser Gln Ile Asp Met Leu Val Pro
505 510 515
cgg cag tgc ttt agc ctg aac tac gac ctg aac tgc gac aag ctg tgc 3560
Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu Asn Cys Asp Lys Leu Cys
520 525 530
gcc gat ttc caa gag gac atc gag ttt cac ttc agc ctc ggc tgg aca 3608
Ala Asp Phe Gln Glu Asp Ile Glu Phe His Phe Ser Leu Gly Trp Thr
535 540 545 550
atg ctg gtc aac aga ttt ctg ggc ccc aag aac agc aga cgg gcc ctg 3656
Met Leu Val Asn Arg Phe Leu Gly Pro Lys Asn Ser Arg Arg Ala Leu
555 560 565
atg ggc tac aac gat cag gtg cag agg ccc att cct ctg aca ccc gcc 3704
Met Gly Tyr Asn Asp Gln Val Gln Arg Pro Ile Pro Leu Thr Pro Ala
570 575 580
aat cct agc atg cct cca ctg cct cag ggc agc ctg aca caa gag gaa 3752
Asn Pro Ser Met Pro Pro Leu Pro Gln Gly Ser Leu Thr Gln Glu Glu
585 590 595
ttc atg gtg tct atg gtc acc ggc ctg gcc agc ctg acc agc aga aca 3800
Phe Met Val Ser Met Val Thr Gly Leu Ala Ser Leu Thr Ser Arg Thr
600 605 610
tct atg ggc atc ctg gtc gtc ggc ggc gtt gtg tgg aaa gct gtt ggc 3848
Ser Met Gly Ile Leu Val Val Gly Gly Val Val Trp Lys Ala Val Gly
615 620 625 630
tgg cgg ctg atc gcc ctg agc ttt ggc ctg tat ggc ctg ctg tac gtg 3896
Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu Tyr Gly Leu Leu Tyr Val
635 640 645
tac gag aga ctg acc tgg acc acc aag gcc aaa gag cgg gcc ttc aag 3944
Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala Lys Glu Arg Ala Phe Lys
650 655 660
cgg cag ttt gtg gaa cac gcc tcc gag aaa ctg cag ctg gtg atc agc 3992
Arg Gln Phe Val Glu His Ala Ser Glu Lys Leu Gln Leu Val Ile Ser
665 670 675
tac acc ggc agc aat tgc agc cac cag gtg cag caa gag ctg tcc gga 4040
Tyr Thr Gly Ser Asn Cys Ser His Gln Val Gln Gln Glu Leu Ser Gly
680 685 690
aca ttc gcc cac ctg tgt cag cag gtc gac gtg acc aga gag aac ctg 4088
Thr Phe Ala His Leu Cys Gln Gln Val Asp Val Thr Arg Glu Asn Leu
695 700 705 710
gaa caa gag atc gcc gcc atg aat aag aaa atc gag gtg ctc gac tcc 4136
Glu Gln Glu Ile Ala Ala Met Asn Lys Lys Ile Glu Val Leu Asp Ser
715 720 725
ctg cag agc aag gcc aag ctg ctg aga aac aag gcc ggc tgg ctg gac 4184
Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn Lys Ala Gly Trp Leu Asp
730 735 740
agc gag ctg aat atg ttc acc cac cag tac ctg cag cct agc cgc taa 4232
Ser Glu Leu Asn Met Phe Thr His Gln Tyr Leu Gln Pro Ser Arg
745 750 755
taaagcggcc gcaagcttgc acccgtacct ttgggagcgc gcgccctcgt cgtgtcgtga 4292
cgtcacccgt tctgttggat ccctggaggc ttgctgaagg ctgtatgctg ttgacgtcca 4352
gaacctgttc tgttttggcc actgactgac agaacaggct ggacgtcaac aggacacaag 4412
gcctgttact agcactcaca tggaacaaat ggcccagatc agctttctag agtcgacccg 4472
ggcggcggcg gccgcctaag gctcgaggat ctttttccct ctgccaaaaa ttatggggac 4532
atcatgaagc cccttgagca tctgacttct ggctaataaa ggaaatttat tttcattgca 4592
atagtgtgtt ggaatttttt gtgtctctca ctcggataag gatcttccta gagcatggct 4652
acgtagataa gtagcatggc gggttaatca ttaactacaa ggaaccccta gtgatggagt 4712
tggccactcc ctctctgcgc gctcgctcgc tcactgaggc cgggcgacca aaggtcgccc 4772
gacgcccggg ctttgcccgg gcggcctcag tgagcgagcg agcgcgcag 4821
<210> 76
<211> 757
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 76
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
Asn Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala
50 55 60
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
Thr Thr Asn Cys Phe Leu Arg Val Glu Gly Thr Asp Gly His Glu Ala
130 135 140
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Arg Ser Ala Lys Thr Val
145 150 155 160
Asn Gln Leu Ala His Ala Leu His Gln Asp Lys Gln Leu His Ala Gly
165 170 175
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys His Phe
225 230 235 240
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
Leu Gly Val Val Asp Arg Ser Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
Ser Ala Lys Glu Val Leu Asn Ala Arg Ile Gln Lys Ala Gln Gly Met
305 310 315 320
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Met Ala Ala Arg
370 375 380
Glu Gln Gln Val Tyr Cys Glu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
Leu Arg Ile Lys Gln Ile Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Asp Tyr
435 440 445
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Ser Gln
500 505 510
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu
515 520 525
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
Ile Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
Ser Leu Thr Gln Glu Glu Phe Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala
645 650 655
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu His Ala Ser Glu Lys
660 665 670
Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
Val Thr Arg Glu Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
Ile Glu Val Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Thr His Gln Tyr
740 745 750
Leu Gln Pro Ser Arg
755
<210> 77
<211> 4905
<212> DNA
<213> Artificial Sequence
<220>
<223> Vector genome CB7.CI.hMfn2.GA.link.miR1518.rBG
<220>
<221> repeat_region
<222> (1)..(130)
<223> ITR
<220>
<221> enhancer
<222> (259)..(562)
<223> CMV enhancer
<220>
<221> promoter
<222> (561)..(842)
<223> CB7 promoter
<220>
<221> Intron
<222> (935)..(1907)
<223> chicken beta-actin intron
<220>
<221> misc_feature
<222> (1953)..(1958)
<223> Kozak
<220>
<221> CDS
<222> (1959)..(4232)
<223> human Mfn2 engineered
<220>
<221> misc_feature
<222> (2174)..(2194)
<223> miR538 mut
<220>
<221> misc_feature
<222> (3329)..(3349)
<223> miR 1518 mutated
<220>
<221> misc_feature
<222> (4233)..(4314)
<223> linker p4271
<220>
<221> misc_feature
<222> (4315)..(4342)
<223> 5' flank
<220>
<221> misc_feature
<222> (4343)..(4363)
<223> rat miR1518 AS
<220>
<221> misc_feature
<222> (4364)..(4382)
<223> loop
<220>
<221> misc_feature
<222> (4383)..(4401)
<223> rat miR 1518 sense
<220>
<221> misc_feature
<222> (4402)..(4446)
<223> 3'Flank
<220>
<221> polyA_signal
<222> (4584)..(4710)
<223> rabbit globin polyA
<220>
<221> repeat_region
<222> (4776)..(4905)
<223> ITR
<400> 77
ctgcgcgctc gctcgctcac tgaggccgcc cgggcaaagc ccgggcgtcg ggcgaccttt 60
ggtcgcccgg cctcagtgag cgagcgagcg cgcagagagg gagtggccaa ctccatcact 120
aggggttcct tgtagttaat gattaacccg ccatgctact tatctacgta gccatgctct 180
aggaagatct gatatcacta gttattaata gtaatcaatt acggggtcat tagttcatag 240
cccatatatg gagttccgcg ttacataact tacggtaaat ggcccgcctg gctgaccgcc 300
caacgacccc cgcccattga cgtcaataat gacgtatgtt cccatagtaa cgccaatagg 360
gactttccat tgacgtcaat gggtggagta tttacggtaa actgcccact tggcagtaca 420
tcaagtgtat catatgccaa gtacgccccc tattgacgtc aatgacggta aatggcccgc 480
ctggcattat gcccagtaca tgaccttatg ggactttcct acttggcagt acatctacgt 540
attagtcatc gctattacca tggtcgaggt gagccccacg ttctgcttca ctctccccat 600
ctcccccccc tccccacccc caattttgta tttatttatt ttttaattat tttgtgcagc 660
gatgggggcg gggggggggg gggggcgcgc gccaggcggg gcggggcggg gcgaggggcg 720
gggcggggcg aggcggagag gtgcggcggc agccaatcag agcggcgcgc tccgaaagtt 780
tccttttatg gcgaggcggc ggcggcggcg gccctataaa aagcgaagcg cgcggcgggc 840
gggagtcgct gcgcgctgcc ttcgccccgt gccccgctcc gccgccgcct cgcgccgccc 900
gccccggctc tgactgaccg cgttactccc acaggtgagc gggcgggacg gcccttctcc 960
tccgggctgt aattagcgct tggtttaatg acggcttgtt tcttttctgt ggctgcgtga 1020
aagccttgag gggctccggg agggcccttt gtgcgggggg agcggctcgg ggggtgcgtg 1080
cgtgtgtgtg tgcgtgggga gcgccgcgtg cggctccgcg ctgcccggcg gctgtgagcg 1140
ctgcgggcgc ggcgcggggc tttgtgcgct ccgcagtgtg cgcgagggga gcgcggccgg 1200
gggcggtgcc ccgcggtgcg gggggggctg cgaggggaac aaaggctgcg tgcggggtgt 1260
gtgcgtgggg gggtgagcag ggggtgtggg cgcgtcggtc gggctgcaac cccccctgca 1320
cccccctccc cgagttgctg agcacggccc ggcttcgggt gcggggctcc gtacggggcg 1380
tggcgcgggg ctcgccgtgc cgggcggggg gtggcggcag gtgggggtgc cgggcggggc 1440
ggggccgcct cgggccgggg agggctcggg ggaggggcgc ggcggccccc ggagcgccgg 1500
cggctgtcga ggcgcggcga gccgcagcca ttgcctttta tggtaatcgt gcgagagggc 1560
gcagggactt cctttgtccc aaatctgtgc ggagccgaaa tctgggaggc gccgccgcac 1620
cccctctagc gggcgcgggg cgaagcggtg cggcgccggc aggaaggaaa tgggcgggga 1680
gggccttcgt gcgtcgccgc gccgccgtcc ccttctccct ctccagcctc ggggctgtcc 1740
gcggggggac ggctgccttc gggggggacg gggcagggcg gggttcggct tctggcgtgt 1800
gaccggcggc tctagagcct ctgctaacca tgttcatgcc ttcttctttt tcctacagct 1860
cctgggcaac gtgctggtta ttgtgctgtc tcatcatttt ggcaaagaat tcacgcgtgc 1920
taggatcccg tacgacgcgt gctagcaccg gtgccacc atg agc ctg ctg ttc agc 1976
Met Ser Leu Leu Phe Ser
1 5
cgg tgc aac agc atc gtg acc gtg aag aaa aac aag cgg cac atg gcc 2024
Arg Cys Asn Ser Ile Val Thr Val Lys Lys Asn Lys Arg His Met Ala
10 15 20
gaa gtg aac gcc tct cca ctg aag cac ttc gtg acc gcc aag aag aag 2072
Glu Val Asn Ala Ser Pro Leu Lys His Phe Val Thr Ala Lys Lys Lys
25 30 35
atc aac ggc atc ttc gag cag ctg ggc gcc tac atc caa gag agc gcc 2120
Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala Tyr Ile Gln Glu Ser Ala
40 45 50
acc ttc ctg gaa gat acc tac aga aac gcc gag ctg gac ccc gtg acc 2168
Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala Glu Leu Asp Pro Val Thr
55 60 65 70
aca gag gaa cag gtg ctg gat gtg aag ggc tac ctg agc aaa gtg cgg 2216
Thr Glu Glu Gln Val Leu Asp Val Lys Gly Tyr Leu Ser Lys Val Arg
75 80 85
ggc atc tct gaa gtg ctg gcc aga cgg cat atg aag gtg gcc ttt ttc 2264
Gly Ile Ser Glu Val Leu Ala Arg Arg His Met Lys Val Ala Phe Phe
90 95 100
ggc cgg acc agc aac ggc aag agc acc gtg atc aat gcc atg ctg tgg 2312
Gly Arg Thr Ser Asn Gly Lys Ser Thr Val Ile Asn Ala Met Leu Trp
105 110 115
gac aaa gtg ctg ccc tct gga atc ggc cac acc acc aac tgc ttt ctg 2360
Asp Lys Val Leu Pro Ser Gly Ile Gly His Thr Thr Asn Cys Phe Leu
120 125 130
aga gtg gaa ggc acc gac ggc cac gag gca ttt ctg ctg aca gag ggc 2408
Arg Val Glu Gly Thr Asp Gly His Glu Ala Phe Leu Leu Thr Glu Gly
135 140 145 150
tcc gag gaa aag cgg agc gcc aag aca gtg aac cag ctg gcc cat gct 2456
Ser Glu Glu Lys Arg Ser Ala Lys Thr Val Asn Gln Leu Ala His Ala
155 160 165
ctg cac cag gat aag cag ctg cat gcc gga agc ctg gtg tcc gtg atg 2504
Leu His Gln Asp Lys Gln Leu His Ala Gly Ser Leu Val Ser Val Met
170 175 180
tgg ccc aat agc aag tgc cct ctg ctg aag gac gac ctg gtg ctg atg 2552
Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys Asp Asp Leu Val Leu Met
185 190 195
gat agc ccc ggg atc gat gtg acc acc gaa ctg gac agc tgg atc gac 2600
Asp Ser Pro Gly Ile Asp Val Thr Thr Glu Leu Asp Ser Trp Ile Asp
200 205 210
aag ttc tgc ctg gac gcc gac gtg ttc gtg ctg gtg gcc aat agc gag 2648
Lys Phe Cys Leu Asp Ala Asp Val Phe Val Leu Val Ala Asn Ser Glu
215 220 225 230
agc acc ctg atg cag acc gag aag cac ttt ttc cac aag gtg tcc gag 2696
Ser Thr Leu Met Gln Thr Glu Lys His Phe Phe His Lys Val Ser Glu
235 240 245
cgg ctg agc aga ccc aat atc ttt atc ctg aac aac aga tgg gac gcc 2744
Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu Asn Asn Arg Trp Asp Ala
250 255 260
agc gcc agc gag ccc gag tat atg gaa gaa gtg cgg cgg cag cat atg 2792
Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu Val Arg Arg Gln His Met
265 270 275
gaa cgg tgc aca tcc ttt ctg gtg gac gag ctg ggc gtc gtg gat aga 2840
Glu Arg Cys Thr Ser Phe Leu Val Asp Glu Leu Gly Val Val Asp Arg
280 285 290
tct cag gcc ggc gac aga atc ttc ttt gtg tcc gcc aaa gag gtg ctg 2888
Ser Gln Ala Gly Asp Arg Ile Phe Phe Val Ser Ala Lys Glu Val Leu
295 300 305 310
aac gcc cgg att cag aaa gcc cag gga atg cct gaa ggc gga ggt gca 2936
Asn Ala Arg Ile Gln Lys Ala Gln Gly Met Pro Glu Gly Gly Gly Ala
315 320 325
ctg gcc gag gga ttt caa gtg cgg atg ttc gag ttc cag aac ttc gag 2984
Leu Ala Glu Gly Phe Gln Val Arg Met Phe Glu Phe Gln Asn Phe Glu
330 335 340
cgg aga ttc gag gag tgc atc agc cag agc gcc gtc aag acc aag ttc 3032
Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser Ala Val Lys Thr Lys Phe
345 350 355
gag cag cat acc gtg cgg gcc aag cag att gcc gaa gcc gtc aga ctg 3080
Glu Gln His Thr Val Arg Ala Lys Gln Ile Ala Glu Ala Val Arg Leu
360 365 370
atc atg gac agc ctg cat atg gcc gcc aga gag cag cag gtc tac tgc 3128
Ile Met Asp Ser Leu His Met Ala Ala Arg Glu Gln Gln Val Tyr Cys
375 380 385 390
gag gaa atg cgg gaa gag aga cag gac cgg ctg aag ttc atc gac aag 3176
Glu Glu Met Arg Glu Glu Arg Gln Asp Arg Leu Lys Phe Ile Asp Lys
395 400 405
cag ctg gaa ctg ctg gcc cag gac tac aag ctg cgg atc aag cag atc 3224
Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys Leu Arg Ile Lys Gln Ile
410 415 420
acc gaa gag gtg gaa aga cag gtg tcc acc gct atg gcc gag gaa atc 3272
Thr Glu Glu Val Glu Arg Gln Val Ser Thr Ala Met Ala Glu Glu Ile
425 430 435
aga cgg ctg agc gtg ctg gtc gac gac tac cag atg gac ttt cac ccc 3320
Arg Arg Leu Ser Val Leu Val Asp Asp Tyr Gln Met Asp Phe His Pro
440 445 450
tct cca gtg gtg ctg aaa gtc tac aaa aac gag ctg cac cgg cac atc 3368
Ser Pro Val Val Leu Lys Val Tyr Lys Asn Glu Leu His Arg His Ile
455 460 465 470
gag gaa ggc ctg ggc aga aac atg agc gac aga tgc agc acc gcc atc 3416
Glu Glu Gly Leu Gly Arg Asn Met Ser Asp Arg Cys Ser Thr Ala Ile
475 480 485
acc aat agc ctg cag acc atg cag cag gac atg atc gac ggc ctg aaa 3464
Thr Asn Ser Leu Gln Thr Met Gln Gln Asp Met Ile Asp Gly Leu Lys
490 495 500
cct ctg ctg cct gtg tcc gtc aga tcc cag atc gat atg ctg gtg ccc 3512
Pro Leu Leu Pro Val Ser Val Arg Ser Gln Ile Asp Met Leu Val Pro
505 510 515
cgg cag tgc ttt agc ctg aac tac gac ctg aac tgc gac aag ctg tgc 3560
Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu Asn Cys Asp Lys Leu Cys
520 525 530
gcc gat ttc caa gag gac atc gag ttt cac ttc agc ctc ggc tgg aca 3608
Ala Asp Phe Gln Glu Asp Ile Glu Phe His Phe Ser Leu Gly Trp Thr
535 540 545 550
atg ctg gtc aac aga ttt ctg ggc ccc aag aac agc aga cgg gcc ctg 3656
Met Leu Val Asn Arg Phe Leu Gly Pro Lys Asn Ser Arg Arg Ala Leu
555 560 565
atg ggc tac aac gat cag gtg cag agg ccc att cct ctg aca ccc gcc 3704
Met Gly Tyr Asn Asp Gln Val Gln Arg Pro Ile Pro Leu Thr Pro Ala
570 575 580
aat cct agc atg cct cca ctg cct cag ggc agc ctg aca caa gag gaa 3752
Asn Pro Ser Met Pro Pro Leu Pro Gln Gly Ser Leu Thr Gln Glu Glu
585 590 595
ttc atg gtg tct atg gtc acc ggc ctg gcc agc ctg acc agc aga aca 3800
Phe Met Val Ser Met Val Thr Gly Leu Ala Ser Leu Thr Ser Arg Thr
600 605 610
tct atg ggc atc ctg gtc gtc ggc ggc gtt gtg tgg aaa gct gtt ggc 3848
Ser Met Gly Ile Leu Val Val Gly Gly Val Val Trp Lys Ala Val Gly
615 620 625 630
tgg cgg ctg atc gcc ctg agc ttt ggc ctg tat ggc ctg ctg tac gtg 3896
Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu Tyr Gly Leu Leu Tyr Val
635 640 645
tac gag aga ctg acc tgg acc acc aag gcc aaa gag cgg gcc ttc aag 3944
Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala Lys Glu Arg Ala Phe Lys
650 655 660
cgg cag ttt gtg gaa cac gcc tcc gag aaa ctg cag ctg gtg atc agc 3992
Arg Gln Phe Val Glu His Ala Ser Glu Lys Leu Gln Leu Val Ile Ser
665 670 675
tac acc ggc agc aat tgc agc cac cag gtg cag caa gag ctg tcc gga 4040
Tyr Thr Gly Ser Asn Cys Ser His Gln Val Gln Gln Glu Leu Ser Gly
680 685 690
aca ttc gcc cac ctg tgt cag cag gtc gac gtg acc aga gag aac ctg 4088
Thr Phe Ala His Leu Cys Gln Gln Val Asp Val Thr Arg Glu Asn Leu
695 700 705 710
gaa caa gag atc gcc gcc atg aat aag aaa atc gag gtg ctc gac tcc 4136
Glu Gln Glu Ile Ala Ala Met Asn Lys Lys Ile Glu Val Leu Asp Ser
715 720 725
ctg cag agc aag gcc aag ctg ctg aga aac aag gcc ggc tgg ctg gac 4184
Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn Lys Ala Gly Trp Leu Asp
730 735 740
agc gag ctg aat atg ttc acc cac cag tac ctg cag cct agc cgc taa 4232
Ser Glu Leu Asn Met Phe Thr His Gln Tyr Leu Gln Pro Ser Arg
745 750 755
taaagcggcc gcaagcttgc acccgtacct ttgggagcgc gcgccctcgt cgtgtcgtga 4292
cgtcacccgt tctgttggat ccctggaggc ttgctgaagg ctgtatgctg ttcttataaa 4352
ccttgaggac agttttggcc actgactgac tgtcctcagt ttataagaac aggacacaag 4412
gcctgttact agcactcaca tggaacaaat ggcccagatc tagggtgggg ccacctgccg 4472
gtaggtgtgc ggtaggcttt tctccgtcgc aggacgcagg gttcgggcct agagcttatc 4532
gttaagcttt ctagagtcga cccgggcggc ggcggccgcc taaggctcga ggatcttttt 4592
ccctctgcca aaaattatgg ggacatcatg aagccccttg agcatctgac ttctggctaa 4652
taaaggaaat ttattttcat tgcaatagtg tgttggaatt ttttgtgtct ctcactcgga 4712
taaggatctt cctagagcat ggctacgtag ataagtagca tggcgggtta atcattaact 4772
acaaggaacc cctagtgatg gagttggcca ctccctctct gcgcgctcgc tcgctcactg 4832
aggccgggcg accaaaggtc gcccgacgcc cgggctttgc ccgggcggcc tcagtgagcg 4892
agcgagcgcg cag 4905
<210> 78
<211> 757
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 78
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
Asn Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala
50 55 60
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
Thr Thr Asn Cys Phe Leu Arg Val Glu Gly Thr Asp Gly His Glu Ala
130 135 140
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Arg Ser Ala Lys Thr Val
145 150 155 160
Asn Gln Leu Ala His Ala Leu His Gln Asp Lys Gln Leu His Ala Gly
165 170 175
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys His Phe
225 230 235 240
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
Leu Gly Val Val Asp Arg Ser Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
Ser Ala Lys Glu Val Leu Asn Ala Arg Ile Gln Lys Ala Gln Gly Met
305 310 315 320
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Met Ala Ala Arg
370 375 380
Glu Gln Gln Val Tyr Cys Glu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
Leu Arg Ile Lys Gln Ile Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Asp Tyr
435 440 445
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Ser Gln
500 505 510
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu
515 520 525
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
Ile Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
Ser Leu Thr Gln Glu Glu Phe Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala
645 650 655
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu His Ala Ser Glu Lys
660 665 670
Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
Val Thr Arg Glu Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
Ile Glu Val Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Thr His Gln Tyr
740 745 750
Leu Gln Pro Ser Arg
755
<210> 79
<211> 4565
<212> DNA
<213> Artificial Sequence
<220>
<223> Vector genome CB7.CI.hMfn2.GA.rBG
<220>
<221> rep_origin
<222> (1)..(130)
<223> ITR
<220>
<221> enhancer
<222> (259)..(562)
<223> CMV enhancer
<220>
<221> promoter
<222> (561)..(842)
<223> CB7 promoter
<220>
<221> TATA_signal
<222> (815)..(818)
<223> TATA signal
<220>
<221> Intron
<222> (935)..(1907)
<223> Chicken beta-actin intron
<220>
<221> misc_feature
<222> (1940)..(1948)
<223> Kozak
<220>
<221> CDS
<222> (1946)..(4219)
<223> huamn Mfn2 engineered
<220>
<221> misc_feature
<222> (2161)..(2181)
<223> miR538 mut
<220>
<221> misc_feature
<222> (3316)..(3336)
<223> miR1518 mutated
<220>
<221> polyA_signal
<222> (4244)..(4370)
<223> rabbit globin polyA
<220>
<221> repeat_region
<222> (4436)..(4565)
<223> ITR
<400> 79
ctgcgcgctc gctcgctcac tgaggccgcc cgggcaaagc ccgggcgtcg ggcgaccttt 60
ggtcgcccgg cctcagtgag cgagcgagcg cgcagagagg gagtggccaa ctccatcact 120
aggggttcct tgtagttaat gattaacccg ccatgctact tatctacgta gccatgctct 180
aggaagatct gatatcacta gttattaata gtaatcaatt acggggtcat tagttcatag 240
cccatatatg gagttccgcg ttacataact tacggtaaat ggcccgcctg gctgaccgcc 300
caacgacccc cgcccattga cgtcaataat gacgtatgtt cccatagtaa cgccaatagg 360
gactttccat tgacgtcaat gggtggagta tttacggtaa actgcccact tggcagtaca 420
tcaagtgtat catatgccaa gtacgccccc tattgacgtc aatgacggta aatggcccgc 480
ctggcattat gcccagtaca tgaccttatg ggactttcct acttggcagt acatctacgt 540
attagtcatc gctattacca tggtcgaggt gagccccacg ttctgcttca ctctccccat 600
ctcccccccc tccccacccc caattttgta tttatttatt ttttaattat tttgtgcagc 660
gatgggggcg gggggggggg gggggcgcgc gccaggcggg gcggggcggg gcgaggggcg 720
gggcggggcg aggcggagag gtgcggcggc agccaatcag agcggcgcgc tccgaaagtt 780
tccttttatg gcgaggcggc ggcggcggcg gccctataaa aagcgaagcg cgcggcgggc 840
gggagtcgct gcgcgctgcc ttcgccccgt gccccgctcc gccgccgcct cgcgccgccc 900
gccccggctc tgactgaccg cgttactccc acaggtgagc gggcgggacg gcccttctcc 960
tccgggctgt aattagcgct tggtttaatg acggcttgtt tcttttctgt ggctgcgtga 1020
aagccttgag gggctccggg agggcccttt gtgcgggggg agcggctcgg ggggtgcgtg 1080
cgtgtgtgtg tgcgtgggga gcgccgcgtg cggctccgcg ctgcccggcg gctgtgagcg 1140
ctgcgggcgc ggcgcggggc tttgtgcgct ccgcagtgtg cgcgagggga gcgcggccgg 1200
gggcggtgcc ccgcggtgcg gggggggctg cgaggggaac aaaggctgcg tgcggggtgt 1260
gtgcgtgggg gggtgagcag ggggtgtggg cgcgtcggtc gggctgcaac cccccctgca 1320
cccccctccc cgagttgctg agcacggccc ggcttcgggt gcggggctcc gtacggggcg 1380
tggcgcgggg ctcgccgtgc cgggcggggg gtggcggcag gtgggggtgc cgggcggggc 1440
ggggccgcct cgggccgggg agggctcggg ggaggggcgc ggcggccccc ggagcgccgg 1500
cggctgtcga ggcgcggcga gccgcagcca ttgcctttta tggtaatcgt gcgagagggc 1560
gcagggactt cctttgtccc aaatctgtgc ggagccgaaa tctgggaggc gccgccgcac 1620
cccctctagc gggcgcgggg cgaagcggtg cggcgccggc aggaaggaaa tgggcgggga 1680
gggccttcgt gcgtcgccgc gccgccgtcc ccttctccct ctccagcctc ggggctgtcc 1740
gcggggggac ggctgccttc gggggggacg gggcagggcg gggttcggct tctggcgtgt 1800
gaccggcggc tctagagcct ctgctaacca tgttcatgcc ttcttctttt tcctacagct 1860
cctgggcaac gtgctggtta ttgtgctgtc tcatcatttt ggcaaagaat tcacgcgtgc 1920
tagcaaggat ccaccggtcg ccacc atg agc ctg ctg ttc agc cgg tgc aac 1972
Met Ser Leu Leu Phe Ser Arg Cys Asn
1 5
agc atc gtg acc gtg aag aaa aac aag cgg cac atg gcc gaa gtg aac 2020
Ser Ile Val Thr Val Lys Lys Asn Lys Arg His Met Ala Glu Val Asn
10 15 20 25
gcc tct cca ctg aag cac ttc gtg acc gcc aag aag aag atc aac gga 2068
Ala Ser Pro Leu Lys His Phe Val Thr Ala Lys Lys Lys Ile Asn Gly
30 35 40
atc ttc gag cag ctg ggc gcc tac atc caa gag agc gcc acc ttc ctg 2116
Ile Phe Glu Gln Leu Gly Ala Tyr Ile Gln Glu Ser Ala Thr Phe Leu
45 50 55
gaa gat acc tac aga aac gcc gag ctg gac ccc gtg acc aca gag gaa 2164
Glu Asp Thr Tyr Arg Asn Ala Glu Leu Asp Pro Val Thr Thr Glu Glu
60 65 70
cag gtg ctg gat gtg aag ggc tac ctg agc aaa gtg cgg ggc atc tct 2212
Gln Val Leu Asp Val Lys Gly Tyr Leu Ser Lys Val Arg Gly Ile Ser
75 80 85
gaa gtg ctg gcc aga cgg cat atg aag gtg gcc ttt ttc ggc cgg acc 2260
Glu Val Leu Ala Arg Arg His Met Lys Val Ala Phe Phe Gly Arg Thr
90 95 100 105
agc aac ggc aag agc acc gtg atc aat gcc atg ctg tgg gac aaa gtg 2308
Ser Asn Gly Lys Ser Thr Val Ile Asn Ala Met Leu Trp Asp Lys Val
110 115 120
ctg ccc tct gga atc ggc cac acc acc aac tgc ttt ctg aga gtg gaa 2356
Leu Pro Ser Gly Ile Gly His Thr Thr Asn Cys Phe Leu Arg Val Glu
125 130 135
ggc acc gac ggc cac gag gca ttt ctg ctg aca gag ggc tcc gag gaa 2404
Gly Thr Asp Gly His Glu Ala Phe Leu Leu Thr Glu Gly Ser Glu Glu
140 145 150
aag cgg agc gcc aag aca gtg aac cag ctg gcc cat gct ctg cac cag 2452
Lys Arg Ser Ala Lys Thr Val Asn Gln Leu Ala His Ala Leu His Gln
155 160 165
gat aag cag ctg cat gcc gga agc ctg gtg tcc gtg atg tgg ccc aat 2500
Asp Lys Gln Leu His Ala Gly Ser Leu Val Ser Val Met Trp Pro Asn
170 175 180 185
agc aag tgc cct ctg ctg aag gac gac ctg gtg ctg atg gat agc ccc 2548
Ser Lys Cys Pro Leu Leu Lys Asp Asp Leu Val Leu Met Asp Ser Pro
190 195 200
ggg atc gat gtg acc acc gaa ctg gac agc tgg atc gac aag ttc tgc 2596
Gly Ile Asp Val Thr Thr Glu Leu Asp Ser Trp Ile Asp Lys Phe Cys
205 210 215
ctg gac gcc gac gtg ttc gtg ctg gtg gcc aat agc gag agc acc ctg 2644
Leu Asp Ala Asp Val Phe Val Leu Val Ala Asn Ser Glu Ser Thr Leu
220 225 230
atg cag acc gag aag cac ttt ttc cac aag gtg tcc gag cgg ctg agc 2692
Met Gln Thr Glu Lys His Phe Phe His Lys Val Ser Glu Arg Leu Ser
235 240 245
aga ccc aat atc ttt atc ctg aac aac aga tgg gac gcc agc gcc agc 2740
Arg Pro Asn Ile Phe Ile Leu Asn Asn Arg Trp Asp Ala Ser Ala Ser
250 255 260 265
gag ccc gag tat atg gaa gaa gtg cgg cgg cag cat atg gaa cgg tgc 2788
Glu Pro Glu Tyr Met Glu Glu Val Arg Arg Gln His Met Glu Arg Cys
270 275 280
aca tcc ttt ctg gtg gac gag ctg ggc gtc gtg gat aga tct cag gcc 2836
Thr Ser Phe Leu Val Asp Glu Leu Gly Val Val Asp Arg Ser Gln Ala
285 290 295
ggc gac aga atc ttc ttt gtg tcc gcc aaa gag gtg ctg aac gcc cgg 2884
Gly Asp Arg Ile Phe Phe Val Ser Ala Lys Glu Val Leu Asn Ala Arg
300 305 310
att cag aaa gcc cag gga atg cct gaa ggc gga ggt gca ctg gcc gag 2932
Ile Gln Lys Ala Gln Gly Met Pro Glu Gly Gly Gly Ala Leu Ala Glu
315 320 325
gga ttt caa gtg cgg atg ttc gag ttc cag aac ttc gag cgg aga ttc 2980
Gly Phe Gln Val Arg Met Phe Glu Phe Gln Asn Phe Glu Arg Arg Phe
330 335 340 345
gag gag tgc atc agc cag agc gcc gtc aag acc aag ttc gag cag cat 3028
Glu Glu Cys Ile Ser Gln Ser Ala Val Lys Thr Lys Phe Glu Gln His
350 355 360
acc gtg cgg gcc aag cag att gcc gaa gcc gtc aga ctg atc atg gac 3076
Thr Val Arg Ala Lys Gln Ile Ala Glu Ala Val Arg Leu Ile Met Asp
365 370 375
agc ctg cat atg gcc gcc aga gag cag cag gtc tac tgc gag gaa atg 3124
Ser Leu His Met Ala Ala Arg Glu Gln Gln Val Tyr Cys Glu Glu Met
380 385 390
cgg gaa gag aga cag gac cgg ctg aag ttc atc gac aag cag ctg gaa 3172
Arg Glu Glu Arg Gln Asp Arg Leu Lys Phe Ile Asp Lys Gln Leu Glu
395 400 405
ctg ctg gcc cag gac tac aag ctg cgg atc aag cag atc acc gaa gag 3220
Leu Leu Ala Gln Asp Tyr Lys Leu Arg Ile Lys Gln Ile Thr Glu Glu
410 415 420 425
gtg gaa aga cag gtg tcc acc gct atg gcc gag gaa atc aga cgg ctg 3268
Val Glu Arg Gln Val Ser Thr Ala Met Ala Glu Glu Ile Arg Arg Leu
430 435 440
agc gtg ctg gtc gac gac tac cag atg gac ttt cac ccc tct cca gtg 3316
Ser Val Leu Val Asp Asp Tyr Gln Met Asp Phe His Pro Ser Pro Val
445 450 455
gtg ctg aaa gtc tac aaa aac gag ctg cac cgg cac atc gag gaa ggc 3364
Val Leu Lys Val Tyr Lys Asn Glu Leu His Arg His Ile Glu Glu Gly
460 465 470
ctg ggc aga aac atg agc gac aga tgc agc acc gcc atc acc aat agc 3412
Leu Gly Arg Asn Met Ser Asp Arg Cys Ser Thr Ala Ile Thr Asn Ser
475 480 485
ctg cag acc atg cag cag gac atg atc gac ggc ctg aaa cct ctg ctg 3460
Leu Gln Thr Met Gln Gln Asp Met Ile Asp Gly Leu Lys Pro Leu Leu
490 495 500 505
cct gtg tcc gtc aga tcc cag atc gat atg ctg gtg ccc cgg cag tgc 3508
Pro Val Ser Val Arg Ser Gln Ile Asp Met Leu Val Pro Arg Gln Cys
510 515 520
ttt agc ctg aac tac gac ctg aac tgc gac aag ctg tgc gcc gat ttc 3556
Phe Ser Leu Asn Tyr Asp Leu Asn Cys Asp Lys Leu Cys Ala Asp Phe
525 530 535
caa gag gac atc gag ttt cac ttc agc ctc ggc tgg aca atg ctg gtc 3604
Gln Glu Asp Ile Glu Phe His Phe Ser Leu Gly Trp Thr Met Leu Val
540 545 550
aac aga ttt ctg ggc ccc aag aac agc aga cgg gcc ctg atg ggc tac 3652
Asn Arg Phe Leu Gly Pro Lys Asn Ser Arg Arg Ala Leu Met Gly Tyr
555 560 565
aac gat cag gtg cag agg ccc att cct ctg aca ccc gcc aat cct agc 3700
Asn Asp Gln Val Gln Arg Pro Ile Pro Leu Thr Pro Ala Asn Pro Ser
570 575 580 585
atg cct cca ctg cct cag ggc agc ctg aca caa gag gaa ttc atg gtg 3748
Met Pro Pro Leu Pro Gln Gly Ser Leu Thr Gln Glu Glu Phe Met Val
590 595 600
tct atg gtc acc ggc ctg gcc agc ctg acc agc aga aca tct atg ggc 3796
Ser Met Val Thr Gly Leu Ala Ser Leu Thr Ser Arg Thr Ser Met Gly
605 610 615
atc ctg gtc gtc ggc ggc gtt gtg tgg aaa gct gtt ggc tgg cgg ctg 3844
Ile Leu Val Val Gly Gly Val Val Trp Lys Ala Val Gly Trp Arg Leu
620 625 630
atc gcc ctg agc ttt ggc ctg tat ggc ctg ctg tac gtg tac gag aga 3892
Ile Ala Leu Ser Phe Gly Leu Tyr Gly Leu Leu Tyr Val Tyr Glu Arg
635 640 645
ctg acc tgg acc acc aag gcc aaa gag cgg gcc ttc aag cgg cag ttt 3940
Leu Thr Trp Thr Thr Lys Ala Lys Glu Arg Ala Phe Lys Arg Gln Phe
650 655 660 665
gtg gaa cac gcc tcc gag aaa ctg cag ctg gtg atc agc tac acc ggc 3988
Val Glu His Ala Ser Glu Lys Leu Gln Leu Val Ile Ser Tyr Thr Gly
670 675 680
agc aat tgc agc cac cag gtg cag caa gag ctg tcc gga aca ttc gcc 4036
Ser Asn Cys Ser His Gln Val Gln Gln Glu Leu Ser Gly Thr Phe Ala
685 690 695
cac ctg tgt cag cag gtc gac gtg acc aga gag aac ctg gaa caa gag 4084
His Leu Cys Gln Gln Val Asp Val Thr Arg Glu Asn Leu Glu Gln Glu
700 705 710
atc gcc gcc atg aat aag aaa atc gag gtg ctc gac tcc ctg cag agc 4132
Ile Ala Ala Met Asn Lys Lys Ile Glu Val Leu Asp Ser Leu Gln Ser
715 720 725
aag gcc aag ctg ctg aga aac aag gcc ggc tgg ctg gac agc gag ctg 4180
Lys Ala Lys Leu Leu Arg Asn Lys Ala Gly Trp Leu Asp Ser Glu Leu
730 735 740 745
aat atg ttc acc cac cag tac ctg cag cct agc cgc taa taaagcggcc 4229
Asn Met Phe Thr His Gln Tyr Leu Gln Pro Ser Arg
750 755
gcctaaggct cgaggatctt tttccctctg ccaaaaatta tggggacatc atgaagcccc 4289
ttgagcatct gacttctggc taataaagga aatttatttt cattgcaata gtgtgttgga 4349
attttttgtg tctctcactc ggataaggat cttcctagag catggctacg tagataagta 4409
gcatggcggg ttaatcatta actacaagga acccctagtg atggagttgg ccactccctc 4469
tctgcgcgct cgctcgctca ctgaggccgg gcgaccaaag gtcgcccgac gcccgggctt 4529
tgcccgggcg gcctcagtga gcgagcgagc gcgcag 4565
<210> 80
<211> 757
<212> PRT
<213> Artificial Sequence
<220>
<223> Synthetic Construct
<400> 80
Met Ser Leu Leu Phe Ser Arg Cys Asn Ser Ile Val Thr Val Lys Lys
1 5 10 15
Asn Lys Arg His Met Ala Glu Val Asn Ala Ser Pro Leu Lys His Phe
20 25 30
Val Thr Ala Lys Lys Lys Ile Asn Gly Ile Phe Glu Gln Leu Gly Ala
35 40 45
Tyr Ile Gln Glu Ser Ala Thr Phe Leu Glu Asp Thr Tyr Arg Asn Ala
50 55 60
Glu Leu Asp Pro Val Thr Thr Glu Glu Gln Val Leu Asp Val Lys Gly
65 70 75 80
Tyr Leu Ser Lys Val Arg Gly Ile Ser Glu Val Leu Ala Arg Arg His
85 90 95
Met Lys Val Ala Phe Phe Gly Arg Thr Ser Asn Gly Lys Ser Thr Val
100 105 110
Ile Asn Ala Met Leu Trp Asp Lys Val Leu Pro Ser Gly Ile Gly His
115 120 125
Thr Thr Asn Cys Phe Leu Arg Val Glu Gly Thr Asp Gly His Glu Ala
130 135 140
Phe Leu Leu Thr Glu Gly Ser Glu Glu Lys Arg Ser Ala Lys Thr Val
145 150 155 160
Asn Gln Leu Ala His Ala Leu His Gln Asp Lys Gln Leu His Ala Gly
165 170 175
Ser Leu Val Ser Val Met Trp Pro Asn Ser Lys Cys Pro Leu Leu Lys
180 185 190
Asp Asp Leu Val Leu Met Asp Ser Pro Gly Ile Asp Val Thr Thr Glu
195 200 205
Leu Asp Ser Trp Ile Asp Lys Phe Cys Leu Asp Ala Asp Val Phe Val
210 215 220
Leu Val Ala Asn Ser Glu Ser Thr Leu Met Gln Thr Glu Lys His Phe
225 230 235 240
Phe His Lys Val Ser Glu Arg Leu Ser Arg Pro Asn Ile Phe Ile Leu
245 250 255
Asn Asn Arg Trp Asp Ala Ser Ala Ser Glu Pro Glu Tyr Met Glu Glu
260 265 270
Val Arg Arg Gln His Met Glu Arg Cys Thr Ser Phe Leu Val Asp Glu
275 280 285
Leu Gly Val Val Asp Arg Ser Gln Ala Gly Asp Arg Ile Phe Phe Val
290 295 300
Ser Ala Lys Glu Val Leu Asn Ala Arg Ile Gln Lys Ala Gln Gly Met
305 310 315 320
Pro Glu Gly Gly Gly Ala Leu Ala Glu Gly Phe Gln Val Arg Met Phe
325 330 335
Glu Phe Gln Asn Phe Glu Arg Arg Phe Glu Glu Cys Ile Ser Gln Ser
340 345 350
Ala Val Lys Thr Lys Phe Glu Gln His Thr Val Arg Ala Lys Gln Ile
355 360 365
Ala Glu Ala Val Arg Leu Ile Met Asp Ser Leu His Met Ala Ala Arg
370 375 380
Glu Gln Gln Val Tyr Cys Glu Glu Met Arg Glu Glu Arg Gln Asp Arg
385 390 395 400
Leu Lys Phe Ile Asp Lys Gln Leu Glu Leu Leu Ala Gln Asp Tyr Lys
405 410 415
Leu Arg Ile Lys Gln Ile Thr Glu Glu Val Glu Arg Gln Val Ser Thr
420 425 430
Ala Met Ala Glu Glu Ile Arg Arg Leu Ser Val Leu Val Asp Asp Tyr
435 440 445
Gln Met Asp Phe His Pro Ser Pro Val Val Leu Lys Val Tyr Lys Asn
450 455 460
Glu Leu His Arg His Ile Glu Glu Gly Leu Gly Arg Asn Met Ser Asp
465 470 475 480
Arg Cys Ser Thr Ala Ile Thr Asn Ser Leu Gln Thr Met Gln Gln Asp
485 490 495
Met Ile Asp Gly Leu Lys Pro Leu Leu Pro Val Ser Val Arg Ser Gln
500 505 510
Ile Asp Met Leu Val Pro Arg Gln Cys Phe Ser Leu Asn Tyr Asp Leu
515 520 525
Asn Cys Asp Lys Leu Cys Ala Asp Phe Gln Glu Asp Ile Glu Phe His
530 535 540
Phe Ser Leu Gly Trp Thr Met Leu Val Asn Arg Phe Leu Gly Pro Lys
545 550 555 560
Asn Ser Arg Arg Ala Leu Met Gly Tyr Asn Asp Gln Val Gln Arg Pro
565 570 575
Ile Pro Leu Thr Pro Ala Asn Pro Ser Met Pro Pro Leu Pro Gln Gly
580 585 590
Ser Leu Thr Gln Glu Glu Phe Met Val Ser Met Val Thr Gly Leu Ala
595 600 605
Ser Leu Thr Ser Arg Thr Ser Met Gly Ile Leu Val Val Gly Gly Val
610 615 620
Val Trp Lys Ala Val Gly Trp Arg Leu Ile Ala Leu Ser Phe Gly Leu
625 630 635 640
Tyr Gly Leu Leu Tyr Val Tyr Glu Arg Leu Thr Trp Thr Thr Lys Ala
645 650 655
Lys Glu Arg Ala Phe Lys Arg Gln Phe Val Glu His Ala Ser Glu Lys
660 665 670
Leu Gln Leu Val Ile Ser Tyr Thr Gly Ser Asn Cys Ser His Gln Val
675 680 685
Gln Gln Glu Leu Ser Gly Thr Phe Ala His Leu Cys Gln Gln Val Asp
690 695 700
Val Thr Arg Glu Asn Leu Glu Gln Glu Ile Ala Ala Met Asn Lys Lys
705 710 715 720
Ile Glu Val Leu Asp Ser Leu Gln Ser Lys Ala Lys Leu Leu Arg Asn
725 730 735
Lys Ala Gly Trp Leu Asp Ser Glu Leu Asn Met Phe Thr His Gln Tyr
740 745 750
Leu Gln Pro Ser Arg
755
<210> 81
<211> 2211
<212> DNA
<213> adeno-associated virus hu68
<220>
<221> CDS
<222> (1)..(2211)
<223> AAVhu68
<400> 81
atg gct gcc gat ggt tat ctt cca gat tgg ctc gag gac aac ctc agt 48
Met Ala Ala Asp Gly Tyr Leu Pro Asp Trp Leu Glu Asp Asn Leu Ser
1 5 10 15
gaa ggc att cgc gag tgg tgg gct ttg aaa cct gga gcc cct caa ccc 96
Glu Gly Ile Arg Glu Trp Trp Ala Leu Lys Pro Gly Ala Pro Gln Pro
20 25 30
aag gca aat caa caa cat caa gac aac gct cgg ggt ctt gtg ctt ccg 144
Lys Ala Asn Gln Gln His Gln Asp Asn Ala Arg Gly Leu Val Leu Pro
35 40 45
ggt tac aaa tac ctt gga ccc ggc aac gga ctc gac aag ggg gag ccg 192
Gly Tyr Lys Tyr Leu Gly Pro Gly Asn Gly Leu Asp Lys Gly Glu Pro
50 55 60
gtc aac gaa gca gac gcg gcg gcc ctc gag cac gac aag gcc tac gac 240
Val Asn Glu Ala Asp Ala Ala Ala Leu Glu His Asp Lys Ala Tyr Asp
65 70 75 80
cag cag ctc aag gcc gga gac aac ccg tac ctc aag tac aac cac gcc 288
Gln Gln Leu Lys Ala Gly Asp Asn Pro Tyr Leu Lys Tyr Asn His Ala
85 90 95
gac gcc gag ttc cag gag cgg ctc aaa gaa gat acg tct ttt ggg ggc 336
Asp Ala Glu Phe Gln Glu Arg Leu Lys Glu Asp Thr Ser Phe Gly Gly
100 105 110
aac ctc ggg cga gca gtc ttc cag gcc aaa aag agg ctt ctt gaa cct 384
Asn Leu Gly Arg Ala Val Phe Gln Ala Lys Lys Arg Leu Leu Glu Pro
115 120 125
ctt ggt ctg gtt gag gaa gcg gct aag acg gct cct gga aag aag agg 432
Leu Gly Leu Val Glu Glu Ala Ala Lys Thr Ala Pro Gly Lys Lys Arg
130 135 140
cct gta gag cag tct cct cag gaa ccg gac tcc tcc gtg ggt att ggc 480
Pro Val Glu Gln Ser Pro Gln Glu Pro Asp Ser Ser Val Gly Ile Gly
145 150 155 160
aaa tcg ggt gca cag ccc gct aaa aag aga ctc aat ttc ggt cag act 528
Lys Ser Gly Ala Gln Pro Ala Lys Lys Arg Leu Asn Phe Gly Gln Thr
165 170 175
ggc gac aca gag tca gtc ccc gac cct caa cca atc gga gaa cct ccc 576
Gly Asp Thr Glu Ser Val Pro Asp Pro Gln Pro Ile Gly Glu Pro Pro
180 185 190
gca gcc ccc tca ggt gtg gga tct ctt aca atg gct tca ggt ggt ggc 624
Ala Ala Pro Ser Gly Val Gly Ser Leu Thr Met Ala Ser Gly Gly Gly
195 200 205
gca cca gtg gca gac aat aac gaa ggt gcc gat gga gtg ggt agt tcc 672
Ala Pro Val Ala Asp Asn Asn Glu Gly Ala Asp Gly Val Gly Ser Ser
210 215 220
tcg gga aat tgg cat tgc gat tcc caa tgg ctg ggg gac aga gtc atc 720
Ser Gly Asn Trp His Cys Asp Ser Gln Trp Leu Gly Asp Arg Val Ile
225 230 235 240
acc acc agc acc cga acc tgg gcc ctg ccc acc tac aac aat cac ctc 768
Thr Thr Ser Thr Arg Thr Trp Ala Leu Pro Thr Tyr Asn Asn His Leu
245 250 255
tac aag caa atc tcc aac agc aca tct gga gga tct tca aat gac aac 816
Tyr Lys Gln Ile Ser Asn Ser Thr Ser Gly Gly Ser Ser Asn Asp Asn
260 265 270
gcc tac ttc ggc tac agc acc ccc tgg ggg tat ttt gac ttc aac aga 864
Ala Tyr Phe Gly Tyr Ser Thr Pro Trp Gly Tyr Phe Asp Phe Asn Arg
275 280 285
ttc cac tgc cac ttc tca cca cgt gac tgg caa aga ctc atc aac aac 912
Phe His Cys His Phe Ser Pro Arg Asp Trp Gln Arg Leu Ile Asn Asn
290 295 300
aac tgg gga ttc cgg cct aag cga ctc aac ttc aag ctc ttc aac att 960
Asn Trp Gly Phe Arg Pro Lys Arg Leu Asn Phe Lys Leu Phe Asn Ile
305 310 315 320
cag gtc aaa gag gtt acg gac aac aat gga gtc aag acc atc gct aat 1008
Gln Val Lys Glu Val Thr Asp Asn Asn Gly Val Lys Thr Ile Ala Asn
325 330 335
aac ctt acc agc acg gtc cag gtc ttc acg gac tca gac tat cag ctc 1056
Asn Leu Thr Ser Thr Val Gln Val Phe Thr Asp Ser Asp Tyr Gln Leu
340 345 350
ccg tac gtg ctc ggg tcg gct cac gag ggc tgc ctc ccg ccg ttc cca 1104
Pro Tyr Val Leu Gly Ser Ala His Glu Gly Cys Leu Pro Pro Phe Pro
355 360 365
gcg gac gtt ttc atg att cct cag tac ggg tat cta acg ctt aat gat 1152
Ala Asp Val Phe Met Ile Pro Gln Tyr Gly Tyr Leu Thr Leu Asn Asp
370 375 380
gga agc caa gcc gtg ggt cgt tcg tcc ttt tac tgc ctg gaa tat ttc 1200
Gly Ser Gln Ala Val Gly Arg Ser Ser Phe Tyr Cys Leu Glu Tyr Phe
385 390 395 400
ccg tcg caa atg cta aga acg ggt aac aac ttc cag ttc agc tac gag 1248
Pro Ser Gln Met Leu Arg Thr Gly Asn Asn Phe Gln Phe Ser Tyr Glu
405 410 415
ttt gag aac gta cct ttc cat agc agc tat gct cac agc caa agc ctg 1296
Phe Glu Asn Val Pro Phe His Ser Ser Tyr Ala His Ser Gln Ser Leu
420 425 430
gac cga ctc atg aat cca ctc atc gac caa tac ttg tac tat ctc tca 1344
Asp Arg Leu Met Asn Pro Leu Ile Asp Gln Tyr Leu Tyr Tyr Leu Ser
435 440 445
aag act att aac ggt tct gga cag aat caa caa acg cta aaa ttc agt 1392
Lys Thr Ile Asn Gly Ser Gly Gln Asn Gln Gln Thr Leu Lys Phe Ser
450 455 460
gtg gcc gga ccc agc aac atg gct gtc cag gga aga aac tac ata cct 1440
Val Ala Gly Pro Ser Asn Met Ala Val Gln Gly Arg Asn Tyr Ile Pro
465 470 475 480
gga ccc agc tac cga caa caa cgt gtc tca acc act gtg act caa aac 1488
Gly Pro Ser Tyr Arg Gln Gln Arg Val Ser Thr Thr Val Thr Gln Asn
485 490 495
aac aac agc gaa ttt gct tgg cct gga gct tct tct tgg gct ctc aat 1536
Asn Asn Ser Glu Phe Ala Trp Pro Gly Ala Ser Ser Trp Ala Leu Asn
500 505 510
gga cgt aat agc ttg atg aat cct gga cct gct atg gcc agc cac aaa 1584
Gly Arg Asn Ser Leu Met Asn Pro Gly Pro Ala Met Ala Ser His Lys
515 520 525
gaa gga gag gac cgt ttc ttt cct ttg tct gga tct tta att ttt ggc 1632
Glu Gly Glu Asp Arg Phe Phe Pro Leu Ser Gly Ser Leu Ile Phe Gly
530 535 540
aaa caa gga act gga aga gac aac gtg gat gcg gac aaa gtc atg ata 1680
Lys Gln Gly Thr Gly Arg Asp Asn Val Asp Ala Asp Lys Val Met Ile
545 550 555 560
acc aac gaa gaa gaa att aaa act acc aac cca gta gca acg gag tcc 1728
Thr Asn Glu Glu Glu Ile Lys Thr Thr Asn Pro Val Ala Thr Glu Ser
565 570 575
tat gga caa gtg gcc aca aac cac cag agt gcc caa gca cag gcg cag 1776
Tyr Gly Gln Val Ala Thr Asn His Gln Ser Ala Gln Ala Gln Ala Gln
580 585 590
acc ggc tgg gtt caa aac caa gga ata ctt ccg ggt atg gtt tgg cag 1824
Thr Gly Trp Val Gln Asn Gln Gly Ile Leu Pro Gly Met Val Trp Gln
595 600 605
gac aga gat gtg tac ctg caa gga ccc att tgg gcc aaa att cct cac 1872
Asp Arg Asp Val Tyr Leu Gln Gly Pro Ile Trp Ala Lys Ile Pro His
610 615 620
acg gac ggc aac ttt cac cct tct ccg ctg atg gga ggg ttt gga atg 1920
Thr Asp Gly Asn Phe His Pro Ser Pro Leu Met Gly Gly Phe Gly Met
625 630 635 640
aag cac ccg cct cct cag atc ctc atc aaa aac aca cct gta cct gcg 1968
Lys His Pro Pro Pro Gln Ile Leu Ile Lys Asn Thr Pro Val Pro Ala
645 650 655
gat cct cca acg gct ttc aac aag gac aag ctg aac tct ttc atc acc 2016
Asp Pro Pro Thr Ala Phe Asn Lys Asp Lys Leu Asn Ser Phe Ile Thr
660 665 670
cag tat tct act ggc caa gtc agc gtg gag att gag tgg gag ctg cag 2064
Gln Tyr Ser Thr Gly Gln Val Ser Val Glu Ile Glu Trp Glu Leu Gln
675 680 685
aag gaa aac agc aag cgc tgg aac ccg gag atc cag tac act tcc aac 2112
Lys Glu Asn Ser Lys Arg Trp Asn Pro Glu Ile Gln Tyr Thr Ser Asn
690 695 700
tat tac aag tct aat aat gtt gaa ttt gct gtt aat act gaa ggt gtt 2160
Tyr Tyr Lys Ser Asn Asn Val Glu Phe Ala Val Asn Thr Glu Gly Val
705 710 715 720
tat tct gaa ccc cgc ccc att ggc acc aga tac ctg act cgt aat ctg 2208
Tyr Ser Glu Pro Arg Pro Ile Gly Thr Arg Tyr Leu Thr Arg Asn Leu
725 730 735
taa 2211
<210> 82
<211> 736
<212> PRT
<213> adeno-associated virus hu68
<400> 82
Met Ala Ala Asp Gly Tyr Leu Pro Asp Trp Leu Glu Asp Asn Leu Ser
1 5 10 15
Glu Gly Ile Arg Glu Trp Trp Ala Leu Lys Pro Gly Ala Pro Gln Pro
20 25 30
Lys Ala Asn Gln Gln His Gln Asp Asn Ala Arg Gly Leu Val Leu Pro
35 40 45
Gly Tyr Lys Tyr Leu Gly Pro Gly Asn Gly Leu Asp Lys Gly Glu Pro
50 55 60
Val Asn Glu Ala Asp Ala Ala Ala Leu Glu His Asp Lys Ala Tyr Asp
65 70 75 80
Gln Gln Leu Lys Ala Gly Asp Asn Pro Tyr Leu Lys Tyr Asn His Ala
85 90 95
Asp Ala Glu Phe Gln Glu Arg Leu Lys Glu Asp Thr Ser Phe Gly Gly
100 105 110
Asn Leu Gly Arg Ala Val Phe Gln Ala Lys Lys Arg Leu Leu Glu Pro
115 120 125
Leu Gly Leu Val Glu Glu Ala Ala Lys Thr Ala Pro Gly Lys Lys Arg
130 135 140
Pro Val Glu Gln Ser Pro Gln Glu Pro Asp Ser Ser Val Gly Ile Gly
145 150 155 160
Lys Ser Gly Ala Gln Pro Ala Lys Lys Arg Leu Asn Phe Gly Gln Thr
165 170 175
Gly Asp Thr Glu Ser Val Pro Asp Pro Gln Pro Ile Gly Glu Pro Pro
180 185 190
Ala Ala Pro Ser Gly Val Gly Ser Leu Thr Met Ala Ser Gly Gly Gly
195 200 205
Ala Pro Val Ala Asp Asn Asn Glu Gly Ala Asp Gly Val Gly Ser Ser
210 215 220
Ser Gly Asn Trp His Cys Asp Ser Gln Trp Leu Gly Asp Arg Val Ile
225 230 235 240
Thr Thr Ser Thr Arg Thr Trp Ala Leu Pro Thr Tyr Asn Asn His Leu
245 250 255
Tyr Lys Gln Ile Ser Asn Ser Thr Ser Gly Gly Ser Ser Asn Asp Asn
260 265 270
Ala Tyr Phe Gly Tyr Ser Thr Pro Trp Gly Tyr Phe Asp Phe Asn Arg
275 280 285
Phe His Cys His Phe Ser Pro Arg Asp Trp Gln Arg Leu Ile Asn Asn
290 295 300
Asn Trp Gly Phe Arg Pro Lys Arg Leu Asn Phe Lys Leu Phe Asn Ile
305 310 315 320
Gln Val Lys Glu Val Thr Asp Asn Asn Gly Val Lys Thr Ile Ala Asn
325 330 335
Asn Leu Thr Ser Thr Val Gln Val Phe Thr Asp Ser Asp Tyr Gln Leu
340 345 350
Pro Tyr Val Leu Gly Ser Ala His Glu Gly Cys Leu Pro Pro Phe Pro
355 360 365
Ala Asp Val Phe Met Ile Pro Gln Tyr Gly Tyr Leu Thr Leu Asn Asp
370 375 380
Gly Ser Gln Ala Val Gly Arg Ser Ser Phe Tyr Cys Leu Glu Tyr Phe
385 390 395 400
Pro Ser Gln Met Leu Arg Thr Gly Asn Asn Phe Gln Phe Ser Tyr Glu
405 410 415
Phe Glu Asn Val Pro Phe His Ser Ser Tyr Ala His Ser Gln Ser Leu
420 425 430
Asp Arg Leu Met Asn Pro Leu Ile Asp Gln Tyr Leu Tyr Tyr Leu Ser
435 440 445
Lys Thr Ile Asn Gly Ser Gly Gln Asn Gln Gln Thr Leu Lys Phe Ser
450 455 460
Val Ala Gly Pro Ser Asn Met Ala Val Gln Gly Arg Asn Tyr Ile Pro
465 470 475 480
Gly Pro Ser Tyr Arg Gln Gln Arg Val Ser Thr Thr Val Thr Gln Asn
485 490 495
Asn Asn Ser Glu Phe Ala Trp Pro Gly Ala Ser Ser Trp Ala Leu Asn
500 505 510
Gly Arg Asn Ser Leu Met Asn Pro Gly Pro Ala Met Ala Ser His Lys
515 520 525
Glu Gly Glu Asp Arg Phe Phe Pro Leu Ser Gly Ser Leu Ile Phe Gly
530 535 540
Lys Gln Gly Thr Gly Arg Asp Asn Val Asp Ala Asp Lys Val Met Ile
545 550 555 560
Thr Asn Glu Glu Glu Ile Lys Thr Thr Asn Pro Val Ala Thr Glu Ser
565 570 575
Tyr Gly Gln Val Ala Thr Asn His Gln Ser Ala Gln Ala Gln Ala Gln
580 585 590
Thr Gly Trp Val Gln Asn Gln Gly Ile Leu Pro Gly Met Val Trp Gln
595 600 605
Asp Arg Asp Val Tyr Leu Gln Gly Pro Ile Trp Ala Lys Ile Pro His
610 615 620
Thr Asp Gly Asn Phe His Pro Ser Pro Leu Met Gly Gly Phe Gly Met
625 630 635 640
Lys His Pro Pro Pro Gln Ile Leu Ile Lys Asn Thr Pro Val Pro Ala
645 650 655
Asp Pro Pro Thr Ala Phe Asn Lys Asp Lys Leu Asn Ser Phe Ile Thr
660 665 670
Gln Tyr Ser Thr Gly Gln Val Ser Val Glu Ile Glu Trp Glu Leu Gln
675 680 685
Lys Glu Asn Ser Lys Arg Trp Asn Pro Glu Ile Gln Tyr Thr Ser Asn
690 695 700
Tyr Tyr Lys Ser Asn Asn Val Glu Phe Ala Val Asn Thr Glu Gly Val
705 710 715 720
Tyr Ser Glu Pro Arg Pro Ile Gly Thr Arg Tyr Leu Thr Arg Asn Leu
725 730 735
<210> 83
<211> 2211
<212> DNA
<213> adeno-associated virus hu68
<400> 83
atggctgccg atggttatct tccagattgg ctcgaggaca acctcagtga aggcattcgc 60
gagtggtggg ctttgaaacc tggagcccct caacccaagg caaatcaaca acatcaagac 120
aacgctcggg gtcttgtgct tccgggttac aaataccttg gacccggcaa cggactcgac 180
aagggggagc cggtcaacga agcagacgcg gcggccctcg agcacgacaa ggcctacgac 240
cagcagctca aggccggaga caacccgtac ctcaagtaca accacgccga cgccgagttc 300
caggagcggc tcaaagaaga tacgtctttt gggggcaacc tcgggcgagc agtcttccag 360
gccaaaaaga ggcttcttga acctcttggt ctggttgagg aagcggctaa gacggctcct 420
ggaaagaaga ggcctgtaga gcagtctcct caggaaccgg actcctccgt gggtattggc 480
aaatcgggtg cacagcccgc taaaaagaga ctcaatttcg gtcagactgg cgacacagag 540
tcagtccccg accctcaacc aatcggagaa cctcccgcag ccccctcagg tgtgggatct 600
cttacaatgg cttcaggtgg tggcgcacca gtggcagaca ataacgaagg tgccgatgga 660
gtgggtagtt cctcgggaaa ttggcattgc gattcccaat ggctggggga cagagtcatc 720
accaccagca cccgaacctg ggccctgccc acctacaaca atcacctcta caagcaaatc 780
tccaacagca catctggagg atcttcaaat gacaacgcct acttcggcta cagcaccccc 840
tgggggtatt ttgacttcaa cagattccac tgccacttct caccacgtga ctggcaaaga 900
ctcatcaaca acaactgggg attccggcct aagcgactca acttcaagct cttcaacatt 960
caggtcaaag aggttacgga caacaatgga gtcaagacca tcgctaataa ccttaccagc 1020
acggtccagg tcttcacgga ctcagactat cagctcccgt acgtgctcgg gtcggctcac 1080
gagggctgcc tcccgccgtt cccagcggac gttttcatga ttcctcagta tggatacctc 1140
accctgaacg acggcagtca ggcggtgggc cgctcatcct tctactgcct ggagtacttc 1200
ccttcgcaga tgctgaggac tggcaacaac ttccagttca gctacgagtt cgagaacgtc 1260
cctttccaca gcagctacgc ccacagccag agtttggacc gcttgatgaa ccctctgatc 1320
gaccagtacc tgtactacct gtcaaagacg atcaacggtt ctggccagaa ccagcagacg 1380
ctgaagttca gcgtggccgg gcctagcaac atggccgtcc agggcagaaa ctacatccct 1440
gggcccagct accggcagca gagagtctca accactgtga ctcagaacaa caacagtgag 1500
ttcgcctggc ctggcgccag ctcttgggcc ctcaacggcc gcaactcgct gatgaaccca 1560
ggcccagcca tggccagtca caaggagggc gaggaccgtt tcttcccttt gtctggctct 1620
ctgatcttcg gcaagcaggg gaccggcaga gacaacgtgg acgcggacaa ggtcatgatc 1680
acgaacgagg aggagatcaa gaccaccaac cctgtggcaa ccgagtccta cggccaggtg 1740
gcaaccaacc accagagcgc ccaggcacag gcgcagactg gctgggtcca gaaccagggg 1800
atcctgcctg gcatggtgtg gcaggaccgt gacgtgtacc tgcagggccc tatctgggca 1860
aagatccctc acacggacgg caacttccac ccttctcctc tgatgggcgg cttcggcatg 1920
aagcacccgc ctcctcagat cctcatcaag aacactccgg tcccggcaga ccctccgacg 1980
gccttcaaca aggacaagct gaactcattc atcactcagt actccactgg ccaggtcagc 2040
gtggagatcg agtgggagct gcagaaggag aacagcaagc gttggaaccc agagatccag 2100
tacacttcca actactacaa gtctaacaac gtggagttcg ccgtcaacac tgagggtgtg 2160
tacagtgagc ctcgccctat cggcacccgg tacctcaccc gaaacttgtg a 2211
<210> 84
<211> 2229
<212> DNA
<213> adeno-associated virus PHP.eB
<220>
<221> CDS
<222> (1)..(2229)
<223> AAV-PHP.eB
<400> 84
atg gct gcc gat ggt tat ctt cca gat tgg ctc gag gac aac ctt agt 48
Met Ala Ala Asp Gly Tyr Leu Pro Asp Trp Leu Glu Asp Asn Leu Ser
1 5 10 15
gaa gga att cgc gag tgg tgg gct ttg aaa cct gga gcc cct caa ccc 96
Glu Gly Ile Arg Glu Trp Trp Ala Leu Lys Pro Gly Ala Pro Gln Pro
20 25 30
aag gca aat caa caa cat caa gac aac gct aga ggt ctt gtg ctt ccg 144
Lys Ala Asn Gln Gln His Gln Asp Asn Ala Arg Gly Leu Val Leu Pro
35 40 45
ggt tac aaa tac ctt gga ccc ggc aac gga ctc gac aag ggg gag ccg 192
Gly Tyr Lys Tyr Leu Gly Pro Gly Asn Gly Leu Asp Lys Gly Glu Pro
50 55 60
gtc aac gca gca gac gcg gcg gcc ctc gag cac gac aaa gcc tac gac 240
Val Asn Ala Ala Asp Ala Ala Ala Leu Glu His Asp Lys Ala Tyr Asp
65 70 75 80
cag cag ctc aag gcc gga gac aac ccg tac ctc aag tac aac cac gcc 288
Gln Gln Leu Lys Ala Gly Asp Asn Pro Tyr Leu Lys Tyr Asn His Ala
85 90 95
gac gcc gag ttc cag gag cgg ctc aaa gaa gat acg tct ttt ggg ggc 336
Asp Ala Glu Phe Gln Glu Arg Leu Lys Glu Asp Thr Ser Phe Gly Gly
100 105 110
aac ctc ggg cga gca gtc ttc cag gcc aaa aag agg ctt ctt gaa cct 384
Asn Leu Gly Arg Ala Val Phe Gln Ala Lys Lys Arg Leu Leu Glu Pro
115 120 125
ctt ggt ctg gtt gag gaa gcg gct aag acg gct cct gga aag aag agg 432
Leu Gly Leu Val Glu Glu Ala Ala Lys Thr Ala Pro Gly Lys Lys Arg
130 135 140
cct gta gag cag tct cct cag gaa ccg gac tcc tcc gcg ggt att ggc 480
Pro Val Glu Gln Ser Pro Gln Glu Pro Asp Ser Ser Ala Gly Ile Gly
145 150 155 160
aaa tcg ggt gca cag ccc gct aaa aag aga ctc aat ttc ggt cag act 528
Lys Ser Gly Ala Gln Pro Ala Lys Lys Arg Leu Asn Phe Gly Gln Thr
165 170 175
ggc gac aca gag tca gtc cca gac cct caa cca atc gga gaa cct ccc 576
Gly Asp Thr Glu Ser Val Pro Asp Pro Gln Pro Ile Gly Glu Pro Pro
180 185 190
gca gcc ccc tca ggt gtg gga tct ctt aca atg gct tca ggt ggt ggc 624
Ala Ala Pro Ser Gly Val Gly Ser Leu Thr Met Ala Ser Gly Gly Gly
195 200 205
gca cca gtg gca gac aat aac gaa ggt gcc gat gga gtg ggt agt tcc 672
Ala Pro Val Ala Asp Asn Asn Glu Gly Ala Asp Gly Val Gly Ser Ser
210 215 220
tcg gga aat tgg cat tgc gat tcc caa tgg ctg ggg gac aga gtc atc 720
Ser Gly Asn Trp His Cys Asp Ser Gln Trp Leu Gly Asp Arg Val Ile
225 230 235 240
acc acc agc acc cga acc tgg gcc ctg ccc acc tac aac aat cac ctc 768
Thr Thr Ser Thr Arg Thr Trp Ala Leu Pro Thr Tyr Asn Asn His Leu
245 250 255
tac aag caa atc tcc aac agc aca tct gga gga tct tca aat gac aac 816
Tyr Lys Gln Ile Ser Asn Ser Thr Ser Gly Gly Ser Ser Asn Asp Asn
260 265 270
gcc tac ttc ggc tac agc acc ccc tgg ggg tat ttt gac ttc aac aga 864
Ala Tyr Phe Gly Tyr Ser Thr Pro Trp Gly Tyr Phe Asp Phe Asn Arg
275 280 285
ttc cac tgc cac ttc tca cca cgt gac tgg cag cga ctc atc aac aac 912
Phe His Cys His Phe Ser Pro Arg Asp Trp Gln Arg Leu Ile Asn Asn
290 295 300
aac tgg gga ttc cgg cct aag cga ctc aac ttc aag ctc ttt aac att 960
Asn Trp Gly Phe Arg Pro Lys Arg Leu Asn Phe Lys Leu Phe Asn Ile
305 310 315 320
cag gtc aaa gag gtt acg gac aac aat gga gtc aag acc atc gcc aat 1008
Gln Val Lys Glu Val Thr Asp Asn Asn Gly Val Lys Thr Ile Ala Asn
325 330 335
aac ctt acc agc acg gtc cag gtc ttc acg gac tca gac tat cag ctc 1056
Asn Leu Thr Ser Thr Val Gln Val Phe Thr Asp Ser Asp Tyr Gln Leu
340 345 350
ccg tac gtg ctc ggg tcg gct cac gag ggc tgc ctc ccg ccg ttc cca 1104
Pro Tyr Val Leu Gly Ser Ala His Glu Gly Cys Leu Pro Pro Phe Pro
355 360 365
gcg gac gtt ttc atg att cct cag tac ggg tat ctg acg ctt aat gat 1152
Ala Asp Val Phe Met Ile Pro Gln Tyr Gly Tyr Leu Thr Leu Asn Asp
370 375 380
gga agc cag gcc gtg ggt cgt tcg tcc ttt tac tgc ctg gaa tat ttc 1200
Gly Ser Gln Ala Val Gly Arg Ser Ser Phe Tyr Cys Leu Glu Tyr Phe
385 390 395 400
ccg tcg caa atg cta aga acg ggt aac aac ttc cag ttc agc tac gag 1248
Pro Ser Gln Met Leu Arg Thr Gly Asn Asn Phe Gln Phe Ser Tyr Glu
405 410 415
ttt gag aac gta cct ttc cat agc agc tac gct cac agc caa agc ctg 1296
Phe Glu Asn Val Pro Phe His Ser Ser Tyr Ala His Ser Gln Ser Leu
420 425 430
gac cga cta atg aat cca ctc atc gac caa tac ttg tac tat ctc tct 1344
Asp Arg Leu Met Asn Pro Leu Ile Asp Gln Tyr Leu Tyr Tyr Leu Ser
435 440 445
aga act att aac ggt tct gga cag aat caa caa acg cta aaa ttc agt 1392
Arg Thr Ile Asn Gly Ser Gly Gln Asn Gln Gln Thr Leu Lys Phe Ser
450 455 460
gtg gcc gga ccc agc aac atg gct gtc cag gga aga aac tac ata cct 1440
Val Ala Gly Pro Ser Asn Met Ala Val Gln Gly Arg Asn Tyr Ile Pro
465 470 475 480
gga ccc agc tac cga caa caa cgt gtc tca acc act gtg act caa aac 1488
Gly Pro Ser Tyr Arg Gln Gln Arg Val Ser Thr Thr Val Thr Gln Asn
485 490 495
aac aac agc gaa ttt gct tgg cct gga gct tct tct tgg gct ctc aat 1536
Asn Asn Ser Glu Phe Ala Trp Pro Gly Ala Ser Ser Trp Ala Leu Asn
500 505 510
gga cgt aat agc ttg atg aat cct gga cct gct atg gcc tct cac aaa 1584
Gly Arg Asn Ser Leu Met Asn Pro Gly Pro Ala Met Ala Ser His Lys
515 520 525
gaa gga gag gac cgt ttc ttt cct ttg tct gga tct tta att ttt ggc 1632
Glu Gly Glu Asp Arg Phe Phe Pro Leu Ser Gly Ser Leu Ile Phe Gly
530 535 540
aaa caa ggt act ggc aga gac aac gtg gat gcg gac aaa gtc atg ata 1680
Lys Gln Gly Thr Gly Arg Asp Asn Val Asp Ala Asp Lys Val Met Ile
545 550 555 560
acc aac gaa gaa gaa att aaa act act aac ccg gta gca acg gag tcc 1728
Thr Asn Glu Glu Glu Ile Lys Thr Thr Asn Pro Val Ala Thr Glu Ser
565 570 575
tat gga caa gtg gcc aca aac cac cag agt gat ggg act ttg gcg gtg 1776
Tyr Gly Gln Val Ala Thr Asn His Gln Ser Asp Gly Thr Leu Ala Val
580 585 590
cct ttt aag gca cag gcg cag acc ggt tgg gtt caa aac caa gga ata 1824
Pro Phe Lys Ala Gln Ala Gln Thr Gly Trp Val Gln Asn Gln Gly Ile
595 600 605
ctt ccg ggt atg gtt tgg cag gac aga gat gtg tac ctg caa gga ccc 1872
Leu Pro Gly Met Val Trp Gln Asp Arg Asp Val Tyr Leu Gln Gly Pro
610 615 620
att tgg gcc aaa att cct cac acg gac ggc aac ttt cac cct tct ccg 1920
Ile Trp Ala Lys Ile Pro His Thr Asp Gly Asn Phe His Pro Ser Pro
625 630 635 640
ctg atg gga ggg ttt gga atg aag cac ccg cct cct cag atc ctc atc 1968
Leu Met Gly Gly Phe Gly Met Lys His Pro Pro Pro Gln Ile Leu Ile
645 650 655
aaa aac aca cct gta cct gcg gat cct cca acg gcc ttc aac aag gac 2016
Lys Asn Thr Pro Val Pro Ala Asp Pro Pro Thr Ala Phe Asn Lys Asp
660 665 670
aag ctg aac tct ttc atc acc cag tat tct act ggt caa gtc agc gtg 2064
Lys Leu Asn Ser Phe Ile Thr Gln Tyr Ser Thr Gly Gln Val Ser Val
675 680 685
gag atc gag tgg gag ctg cag aag gaa aac agc aag cgc tgg aac ccg 2112
Glu Ile Glu Trp Glu Leu Gln Lys Glu Asn Ser Lys Arg Trp Asn Pro
690 695 700
gag atc cag tac act tcc aac tat tac aag tct aat aat gtt gaa ttt 2160
Glu Ile Gln Tyr Thr Ser Asn Tyr Tyr Lys Ser Asn Asn Val Glu Phe
705 710 715 720
gct gtt aat act gaa ggt gta tat agt gaa ccc cgc ccc att ggc acc 2208
Ala Val Asn Thr Glu Gly Val Tyr Ser Glu Pro Arg Pro Ile Gly Thr
725 730 735
aga tac ctg act cgt aat ctg 2229
Arg Tyr Leu Thr Arg Asn Leu
740
<210> 85
<211> 743
<212> PRT
<213> adeno-associated virus PHP.eB
<400> 85
Met Ala Ala Asp Gly Tyr Leu Pro Asp Trp Leu Glu Asp Asn Leu Ser
1 5 10 15
Glu Gly Ile Arg Glu Trp Trp Ala Leu Lys Pro Gly Ala Pro Gln Pro
20 25 30
Lys Ala Asn Gln Gln His Gln Asp Asn Ala Arg Gly Leu Val Leu Pro
35 40 45
Gly Tyr Lys Tyr Leu Gly Pro Gly Asn Gly Leu Asp Lys Gly Glu Pro
50 55 60
Val Asn Ala Ala Asp Ala Ala Ala Leu Glu His Asp Lys Ala Tyr Asp
65 70 75 80
Gln Gln Leu Lys Ala Gly Asp Asn Pro Tyr Leu Lys Tyr Asn His Ala
85 90 95
Asp Ala Glu Phe Gln Glu Arg Leu Lys Glu Asp Thr Ser Phe Gly Gly
100 105 110
Asn Leu Gly Arg Ala Val Phe Gln Ala Lys Lys Arg Leu Leu Glu Pro
115 120 125
Leu Gly Leu Val Glu Glu Ala Ala Lys Thr Ala Pro Gly Lys Lys Arg
130 135 140
Pro Val Glu Gln Ser Pro Gln Glu Pro Asp Ser Ser Ala Gly Ile Gly
145 150 155 160
Lys Ser Gly Ala Gln Pro Ala Lys Lys Arg Leu Asn Phe Gly Gln Thr
165 170 175
Gly Asp Thr Glu Ser Val Pro Asp Pro Gln Pro Ile Gly Glu Pro Pro
180 185 190
Ala Ala Pro Ser Gly Val Gly Ser Leu Thr Met Ala Ser Gly Gly Gly
195 200 205
Ala Pro Val Ala Asp Asn Asn Glu Gly Ala Asp Gly Val Gly Ser Ser
210 215 220
Ser Gly Asn Trp His Cys Asp Ser Gln Trp Leu Gly Asp Arg Val Ile
225 230 235 240
Thr Thr Ser Thr Arg Thr Trp Ala Leu Pro Thr Tyr Asn Asn His Leu
245 250 255
Tyr Lys Gln Ile Ser Asn Ser Thr Ser Gly Gly Ser Ser Asn Asp Asn
260 265 270
Ala Tyr Phe Gly Tyr Ser Thr Pro Trp Gly Tyr Phe Asp Phe Asn Arg
275 280 285
Phe His Cys His Phe Ser Pro Arg Asp Trp Gln Arg Leu Ile Asn Asn
290 295 300
Asn Trp Gly Phe Arg Pro Lys Arg Leu Asn Phe Lys Leu Phe Asn Ile
305 310 315 320
Gln Val Lys Glu Val Thr Asp Asn Asn Gly Val Lys Thr Ile Ala Asn
325 330 335
Asn Leu Thr Ser Thr Val Gln Val Phe Thr Asp Ser Asp Tyr Gln Leu
340 345 350
Pro Tyr Val Leu Gly Ser Ala His Glu Gly Cys Leu Pro Pro Phe Pro
355 360 365
Ala Asp Val Phe Met Ile Pro Gln Tyr Gly Tyr Leu Thr Leu Asn Asp
370 375 380
Gly Ser Gln Ala Val Gly Arg Ser Ser Phe Tyr Cys Leu Glu Tyr Phe
385 390 395 400
Pro Ser Gln Met Leu Arg Thr Gly Asn Asn Phe Gln Phe Ser Tyr Glu
405 410 415
Phe Glu Asn Val Pro Phe His Ser Ser Tyr Ala His Ser Gln Ser Leu
420 425 430
Asp Arg Leu Met Asn Pro Leu Ile Asp Gln Tyr Leu Tyr Tyr Leu Ser
435 440 445
Arg Thr Ile Asn Gly Ser Gly Gln Asn Gln Gln Thr Leu Lys Phe Ser
450 455 460
Val Ala Gly Pro Ser Asn Met Ala Val Gln Gly Arg Asn Tyr Ile Pro
465 470 475 480
Gly Pro Ser Tyr Arg Gln Gln Arg Val Ser Thr Thr Val Thr Gln Asn
485 490 495
Asn Asn Ser Glu Phe Ala Trp Pro Gly Ala Ser Ser Trp Ala Leu Asn
500 505 510
Gly Arg Asn Ser Leu Met Asn Pro Gly Pro Ala Met Ala Ser His Lys
515 520 525
Glu Gly Glu Asp Arg Phe Phe Pro Leu Ser Gly Ser Leu Ile Phe Gly
530 535 540
Lys Gln Gly Thr Gly Arg Asp Asn Val Asp Ala Asp Lys Val Met Ile
545 550 555 560
Thr Asn Glu Glu Glu Ile Lys Thr Thr Asn Pro Val Ala Thr Glu Ser
565 570 575
Tyr Gly Gln Val Ala Thr Asn His Gln Ser Asp Gly Thr Leu Ala Val
580 585 590
Pro Phe Lys Ala Gln Ala Gln Thr Gly Trp Val Gln Asn Gln Gly Ile
595 600 605
Leu Pro Gly Met Val Trp Gln Asp Arg Asp Val Tyr Leu Gln Gly Pro
610 615 620
Ile Trp Ala Lys Ile Pro His Thr Asp Gly Asn Phe His Pro Ser Pro
625 630 635 640
Leu Met Gly Gly Phe Gly Met Lys His Pro Pro Pro Gln Ile Leu Ile
645 650 655
Lys Asn Thr Pro Val Pro Ala Asp Pro Pro Thr Ala Phe Asn Lys Asp
660 665 670
Lys Leu Asn Ser Phe Ile Thr Gln Tyr Ser Thr Gly Gln Val Ser Val
675 680 685
Glu Ile Glu Trp Glu Leu Gln Lys Glu Asn Ser Lys Arg Trp Asn Pro
690 695 700
Glu Ile Gln Tyr Thr Ser Asn Tyr Tyr Lys Ser Asn Asn Val Glu Phe
705 710 715 720
Ala Val Asn Thr Glu Gly Val Tyr Ser Glu Pro Arg Pro Ile Gly Thr
725 730 735
Arg Tyr Leu Thr Arg Asn Leu
740
<210> 86
<211> 841
<212> DNA
<213> Artificial Sequence
<220>
<223> CB7 Promoter with CMV enhancer
<400> 86
ccattgacgt caataatgac gtatgttccc atagtaacgc caatagggac tttccattga 60
cgtcaatggg tggagtattt acggtaaact gcccacttgg cagtacatca agtgtatcat 120
atgccaagta cgccccctat tgacgtcaat gacggtaaat ggcccgcctg gcattatgcc 180
cagtacatga ccttatggga ctttcctact tggcagtaca tctacgtatt agtcatcgct 240
attaccatgg tcgaggtgag ccccacgttc tgcttcactc tccccatctc ccccccctcc 300
ccacccccaa ttttgtattt atttattttt taattatttt gtgcagcgat gggggcgggg 360
gggggggggg ggcgcgcgcc aggcggggcg gggcggggcg aggggcgggg cggggcgagg 420
cggagaggtg cggcggcagc caatcagagc ggcgcgctcc gaaagtttcc ttttatggcg 480
aggcggcggc ggcggcggcc ctataaaaag cgaagcgcgc ggcgggcggg agtcgctgcg 540
cgctgccttc gccccgtgcc ccgctccgcc gccgcctcgc gccgcccgcc ccggctctga 600
ctgaccgcgt tactcccaca ggtgagcggg cgggacggcc cttctcctcc gggctgtaat 660
tagcgcttgg tttaatgacg gcttgtttct tttctgtggc tgcgtgaaag ccttgagggg 720
ctccgggagg gccctttgtg cggggggagc ggctcggggc tgtccgcggg gggacggctg 780
ccttcggggg ggacggggca gggcggggtt cggcttctgg cgtgtgaccg gcggctctag 840
a 841
<210> 87
<211> 841
<212> DNA
<213> Artificial Sequence
<220>
<223> CAG promoter
<400> 87
ccattgacgt caataatgac gtatgttccc atagtaacgc caatagggac tttccattga 60
cgtcaatggg tggagtattt acggtaaact gcccacttgg cagtacatca agtgtatcat 120
atgccaagta cgccccctat tgacgtcaat gacggtaaat ggcccgcctg gcattatgcc 180
cagtacatga ccttatggga ctttcctact tggcagtaca tctacgtatt agtcatcgct 240
attaccatgg tcgaggtgag ccccacgttc tgcttcactc tccccatctc ccccccctcc 300
ccacccccaa ttttgtattt atttattttt taattatttt gtgcagcgat gggggcgggg 360
gggggggggg ggcgcgcgcc aggcggggcg gggcggggcg aggggcgggg cggggcgagg 420
cggagaggtg cggcggcagc caatcagagc ggcgcgctcc gaaagtttcc ttttatggcg 480
aggcggcggc ggcggcggcc ctataaaaag cgaagcgcgc ggcgggcggg agtcgctgcg 540
cgctgccttc gccccgtgcc ccgctccgcc gccgcctcgc gccgcccgcc ccggctctga 600
ctgaccgcgt tactcccaca ggtgagcggg cgggacggcc cttctcctcc gggctgtaat 660
tagcgcttgg tttaatgacg gcttgtttct tttctgtggc tgcgtgaaag ccttgagggg 720
ctccgggagg gccctttgtg cggggggagc ggctcggggc tgtccgcggg gggacggctg 780
ccttcggggg ggacggggca gggcggggtt cggcttctgg cgtgtgaccg gcggctctag 840
a 841
<210> 88
<211> 127
<212> DNA
<213> Artificial Sequence
<220>
<223> rabbit beta-globin
<400> 88
gatctttttc cctctgccaa aaattatggg gacatcatga agccccttga gcatctgact 60
tctggctaat aaaggaaatt tattttcatt gcaatagtgt gttggaattt tttgtgtctc 120
tcactcg 127
<210> 89
<211> 59
<212> DNA
<213> Artificial Sequence
<220>
<223> miR1538
<400> 89
ttgacgtcca gaacctgttc tgttttggcc actgactgac agaacaggct ggacgtcaa 59
<210> 90
<211> 82
<212> DNA
<213> Artificial Sequence
<220>
<223> linker
<400> 90
taaagcggcc gcaagcttgc acccgtacct ttgggagcgc gcgccctcgt cgtgtcgtga 60
cgtcacccgt tctgttggat cc 82
Claims (49)
- 재조합 아데노-연관 바이러스(rAAV)로서, AAV 캡시드 및 내부에 패키징된 벡터 게놈을 포함하며, 상기 벡터 게놈은
(a) 인간 미토푸신 2(hMfn2)를 암호화하는 조작된 핵산 서열;
(b) (a)와 (c) 사이에 위치한 스페이서 서열;
(c) CMT2 환자의 내인성 인간 미토푸신 2 핵산 서열 내의 표적 부위에 특이적인 적어도 하나의 miRNA 암호화 서열; 및
(d) (a) 및 (c)에 작동가능하게 연결된 조절 서열로서, 세포에서 이의 발현을 지시하는, 조절 서열
을 포함하며, 상기 (a)의 조작된 핵산 서열은 (c)의 적어도 하나의 miRNA에 대한 표적 부위가 결여되어, 적어도 하나의 miRNA가 조작된 hMfn2 암호화 서열을 표적화하는 것을 방지하는, 재조합 아데노-연관 바이러스(rAAV). - 제1항에 있어서, 상기 AAV 캡시드는 AAVrh91, AAV9, AAV9.PHP.eB, AAVhu68, 또는 AAV1 캡시드로부터 선택되는 것인, rAAV.
- 제1항 또는 제2항에 있어서, 상기 조작된 hMfn2 암호화 서열은 서열번호 11의 핵산 서열 또는 이와 적어도 90% 동일한 서열을 갖는 것인, rAAV.
- 제1항 내지 제3항에 있어서, 상기 조작된 hMfn2 암호화 서열은 서열번호 11의 핵산 서열 또는 이와 적어도 약 80% 동일한 서열을 가지며, 상기 조작된 hMfn2 암호화 서열의 nt 216 내지 236 및/또는 nt 1371 내지 1391은 보존되는 것인, rAAV.
- 제1항 내지 제4항 중 어느 한 항에 있어서, 상기 적어도 하나의 miRNA는 서열번호 89 (miR538, 59 nt)를 포함하는 서열 또는 서열번호 89와 적어도 99% 동일한 서열을 표적화하는 miRNA, 또는 AGAACAGGTTCTGGACGTCAA, 서열번호 27의 안티센스 서열 중 하나 이상을 포함하는 miRNA 중 하나 이상의 서열을 포함하며, 상기 적어도 하나의 miRNA는 (a)의 조작된 hMfn2 암호화 서열 또는 이의 암호화된 메신저 RNA (mRNA)에 결합하지 않는 것인, rAAV.
- 제1항 내지 제4항 중 어느 한 항에 있어서, 상기 적어도 하나의 miRNA 암호화 서열은 서열번호 15 (miR1693, 64 nt)를 포함하는 서열을 표적화하는 miRNA, AAACCTTGAGGACTACTGGAG, 서열번호 32의 안티센스 서열 중 하나 이상을 포함하는 miRNA, 또는 서열번호 16 (miR1518, 59 nt)을 포함하는 서열 또는 서열번호 16과 적어도 99% 동일성인 서열을 표적화하는 miRNA 중 하나 이상의 서열을 포함하며, 상기 적어도 하나의 miRNA는 (a)의 조작된 hMfn2 암호화 서열 또는 이의 암호화된 mRNA에 결합하지 않는 것인, rAAV.
- 제1항 내지 제6항 중 어느 한 항에 있어서, 상기 스페이서는 길이가 75개의 뉴클레오타이드 내지 약 250개의 뉴클레오타이드인, rAAV.
- 제1항 내지 제7항 중 어느 한 항에 있어서, 상기 적어도 하나의 miRNA 암호화 서열은 조작된 hMfn2 암호화 서열에 대해 3'인, rAAV.
- 제1항 내지 제7항 중 어느 한 항에 있어서, 상기 적어도 하나의 miRNA 암호화 서열은 인트론 서열 내에 위치하는 것인, rAAV.
- 제1항 내지 제9항 중 어느 한 항에 있어서, 상기 적어도 하나의 miRNA 암호화 서열은 하나 이상의 miRNA 암호화 서열을 추가로 포함하는 것인, rAAV.
- 제1항 내지 10항 중 어느 한 항에 있어서, 상기 벡터 게놈은 구성적 프로모터, 선택적으로 CB7 프로모터 또는 CAG 프로모터를 추가로 포함하는 것인, rAAV.
- 제1항 내지 10항 중 어느 한 항에 있어서, 상기 벡터 게놈은 인간 시냅신(hSyn) 프로모터인 조직 특이적 프로모터를 추가로 포함하는 것인, rAAV.
- (a) 인간 미토푸신 2(hMfn2)를 암호화하는 조작된 핵산 서열로서, 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결된, 조작된 핵산 서열; 및/또는
(b) 조작된 hMfn2 암호화 서열에 존재하지 않는 내인성 인간 미토푸신 2 암호화 서열의 mRNA 상의 부위를 특이적으로 표적화함으로써 내인성 인간 미토푸신 2의 발현을 억제하는 miRNA를 형성하는 적어도 하나의 헤어핀을 암호화하는 핵산 서열로서, 상기 적어도 하나의 헤어핀 miRNA 암호화 서열은 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되어, 적어도 하나의 헤어핀 miRNA가 조작된 hMfn2 암호화 서열로부터 발현을 감소시키는 것을 방지하는, 핵산 서열
을 포함하는 벡터로서,
상기 (a)의 조작된 hMfn2 암호화 서열은 (b)에 의해 암호화된 적어도 하나의 헤어핀 miRNA에 대한 표적 부위가 결여되어 있는, 벡터. - 제13항에 있어서, 상기 벡터는 조작된 hMfn2 암호화 서열, 하나 이상의 miRNA 암호화 서열 또는 하나 이상의 인공 miRNA(AmiRNA) 암호화 서열인 적어도 하나의 헤어핀 miRNA 암호화 서열, 및 조절 서열을 포함하는 복제-결함성 바이러스 벡터인, 벡터.
- 제14항에 있어서, 상기 바이러스 벡터는 조작된 hMfn2 암호화 서열, 적어도 하나의 헤어핀 miRNA 암호화 서열 및 조절 서열을 포함하는 벡터 게놈이 내부에 패키징된 AAV 캡시드를 갖는 재조합 아데노-연관 바이러스(rAAV) 입자인, 벡터.
- 제15항에 있어서, 상기 AAV 캡시드는 AAVrh91 캡시드, AAV9, AAV9.PHB.eB, AAVhu68, 또는 AAV1로부터 선택되는 것인, 벡터.
- 제13항 내지 16항 중 어느 한 항에 있어서, 상기 조작된 hMfn2 암호화 서열은 서열번호 11의 핵산 서열 또는 서열번호 11과 적어도 90% 동일한 서열을 갖는 것인, 벡터.
- 제13항 내지 17항에 있어서, 상기 조작된 hMfn2 암호화 서열은 서열번호 11의 핵산 서열 또는 서열번호 11과 적어도 80% 동일한 서열을 가지며, 상기 조작된 hMfn2 암호화 서열의 nt 216 내지 236 및/또는 nt 1371 내지 1391은 보존되는 것인, 벡터.
- 제13항 내지 18항 중 어느 한 항에 있어서, 상기 적어도 하나의 헤어핀 miRNA는 miR538이고, 이의 암호화 서열은 서열번호 89의 서열 또는 서열번호 89와 적어도 99% 동일한 서열의 핵산 서열을 포함하며, 상기 적어도 하나의 헤어핀 miRNA는 (a)의 조작된 hMfn2 암호화 서열 또는 이의 암호화된 mRNA에 결합하지 않는 것인, 벡터.
- 제13항 내지 18항 중 어느 한 항에 있어서, 상기 적어도 하나의 헤어핀 miRNA 암호화 서열은,
(a) 서열번호 15 (miR1693, 64 nt);
(b) 서열번호 15의 적어도 60개의 연속적인 뉴클레오타이드;
(c) 서열번호 15와 적어도 99% 동일성으로서, 서열번호 15 (또는 서열번호 68)의 약 6개의 뉴클레오타이드 내지 약 26개의 뉴클레오타이드와 100% 동일성을 갖는 서열을 포함하는, 동일성;
(d) 하기 중 하나 이상의 시드 서열을 포함하는 헤어핀 miRNA 암호화 서열:
(i) TTGACGTCCAGAACCTGTTCT, 서열번호 27;
(ii) AGAAGTGGGCACTTAGAGTTG, 서열번호 28;
(iii) TTCAGAAGTGGGCACTTAGAG, 서열번호 29;
(iv) TTGTCAATCCAGCTGTCCAGC, 서열번호 30;
(v) CAAACTTGGTCTTCACTGCAG, 서열번호 31;
(vi) AAACCTTGAGGACTACTGGAG, 서열번호 32;
(vii) TAACCATGGAAACCATGAACT, 서열번호 33;
(viii) ACAACAAGAATGCCCATGGAG, 서열번호 34;
(ix) AAAGGTCCCAGACAGTTCCTG, 서열번호 35;
(x) TGTTCATGGCGGCAATTTCCT, 서열번호 36;
(xi) TGAGGTTGGCTATTGATTGAC, 서열번호 37;
(xii) TTCTCACACAGTCAACACCTT, 서열번호 38;
(xiii) TTTCCTCGCAGTAAACCTGCT, 서열번호 39;
(xiv) AGAAATGGAACTCAATGTCTT, 서열번호 40;
(xv) TGAACAGGACATCACCTGTGA, 서열번호 41;
(xvi) AATACAAGCAGGTATGTGAAC, 서열번호 42;
(xvii) TAAACCTGCTGCTCCCGAGCC, 서열번호 43;
(xviii) TAGAGGAGGCCATAGAGCCCA, 서열번호 44;
(xix) TCTACCCGCAGGAAGCAATTG, 서열번호 45; 또는
(xx) CTCCTTAGCAGACACAAAGAA, 서열번호 46, 또는 (i) 내지 (xx) 중 임의의 조합
중 하나 이상의 서열을 포함하며,
상기 헤어핀 miRNA는 조작된 hMfn2 암호화 서열 또는 이의 암호화된 mRNA에 결합하지 않는 것인, 벡터. - 제13항 내지 제20항 중 어느 한 항에 있어서, 단일 핵산 분자에 조작된 hMfn2 암호화 서열 및 적어도 하나의 miRNA 암호화 서열을 포함하고, 조작된 hMfn2 암호화 서열과 적어도 하나의 miRNA 암호화 서열 사이에 적어도 75개의 뉴클레오타이드의 스페이서를 추가로 포함하는, 벡터.
- 제13항 내지 제21항 중 어느 한 항에 있어서, 상기 miRNA 암호화 서열은 조작된 hMfn2 암호화 서열에 대해 3'인, 벡터.
- 제13항 내지 제21항 중 어느 한 항에 있어서, 상기 miRNA 암호화 서열은 인트론 서열 내에 위치하는 것인, 벡터.
- 제13항 내지 제23항 중 어느 한 항에 있어서, 하나 이상의 miRNA 암호화 서열을 추가로 포함하는 것인, 벡터.
- 제13항 내지 제24항 중 어느 한 항에 있어서, 상기 조절 서열은 구성적 프로모터, 선택적으로 CB7 프로모터 또는 CAG 프로모터를 포함하는 것인, 벡터.
- 제13항 내지 제24항 중 어느 한 항에 있어서, 상기 조절 서열은 뉴런 특이적 프로모터, 선택적으로 인간 시냅신 프로모터를 포함하는 것인, 벡터.
- 제13항에 있어서, 상기 벡터는 비-바이러스 벡터인, 벡터.
- 제27항에 있어서, 상기 적어도 하나의 비-바이러스 벡터는 리포좀인, 벡터.
- 제13항, 제14항 또는 제17항 내지 제26항 중 어느 한 항에 있어서, 상기 벡터는 재조합 파르보바이러스, 재조합 렌티바이러스, 또는 재조합 단순 헤르페스 바이러스로부터 선택되는 복제-불능, 재조합 바이러스 벡터인, 벡터.
- 서열번호 11의 핵산 서열 또는 서열번호 11과 적어도 90% 동일한 서열을 갖는 조작된 인간 미토푸신 2(hMfn2) 암호화 서열을 포함하고, 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되는 것인, 벡터.
- 제30항에 있어서, 재조합 아데노-연관 바이러스, 재조합 렌티바이러스, 또는 재조합 단순 헤르페스 바이러스로부터 선택되는 복제-결함성 바이러스 벡터인, 벡터.
- 제31항에 있어서, 상기 바이러스 벡터는 조작된 hMfn2 암호화 서열 및 조절 서열을 포함하는 벡터 게놈이 내부에 패키징된 AAV 캡시드를 갖는 재조합 아데노-연관 바이러스(rAAV) 입자인, 벡터.
- 제32항에 있어서, 상기 AAV 캡시드는 AAVrh91, AAV9, AAV9.PHP.eB, AAVhu68, 또는 AAV1 캡시드로부터 선택되는 것인, 벡터.
- 제13항 내지 제17항에 있어서, 상기 조작된 hMfn2 암호화 서열은 서열번호 11의 핵산 서열을 갖고, CB7 프로모터를 추가로 포함하는 것인, 벡터.
- 제13항 내지 제17항에 있어서, 상기 조작된 hMfn2 암호화 서열은 서열번호 11의 핵산 서열을 갖고, 인간 시냅신(hSyn) 프로모터를 추가로 포함하는 것인, 벡터.
- 제13항 내지 제17항에 있어서, 상기 조작된 hMfn2 암호화 서열은 서열번호 11의 핵산 서열을 갖고, CAG 프로모터를 추가로 포함하는 것인, 벡터.
- 조작된 인간 미토푸신 2 (hMfn2) 암호화 서열을 포함하는 재조합 핵산 서열 및 샤르코-마리-투스 2A(CMT2A) 환자의 내인성 인간 미토푸신 2 핵산 서열 내의 표적 부위에 특이적인 적어도 하나의 miRNA를 포함하는 조성물로서, 조작된 인간 미토푸신 2 (hMfn2) 암호화 서열은 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되고, 적어도 하나의 miRNA는 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되며, 상기 조작된 hMfn2 암호화 서열은 적어도 하나의 miRNA에 대한 표적 부위가 결여되어, miRNA가 조작된 Mfn2 암호화 서열을 표적화하는 것을 방지하는, 조성물.
- 제1항 내지 제12항 중 어느 한 항에 따른 rAAV, 제13항 내지 제36항 중 어느 한 항에 따른 벡터, 또는 제37항에 따른 조성물, 및 약제학적으로 허용가능한 수성 현탁액, 부형제, 및/또는 희석제를 포함하는, 약제학적 조성물.
- 샤르코-마리-투스 2A(CMT2A) 신경병증을 갖는 환자를 치료하는 방법으로서, 유효량의 제1항 내지 제12항 중 어느 한 항에 따른 재조합 AAV, 제13항 내지 제36항 중 어느 한 항에 따른 벡터, 또는 제37항에 따른 조성물을 이를 필요로 하는 환자에게 전달하는 것을 포함하는, 방법.
- 샤르코-마리-투스 2A(CMT2A) 신경병증을 갖는 환자에서 신경병증을 감소시키는 방법으로서, 유효량의 제1항 내지 제12항 중 어느 한 항에 따른 재조합 AAV, 제13항 내지 제36항 중 어느 한 항에 따른 벡터, 또는 제37항에 따른 조성물을 이를 필요로 하는 환자에게 전달하는 것을 포함하는, 방법.
- 샤르코-마리-투스 2A(CMT2A) 질환 또는 신경병증을 갖는 환자의 치료에 적합한 제1항 내지 제12항 중 어느 한 항에 따른 재조합 AAV, 제13항 내지 제36항 중 어느 한 항에 따른 벡터, 또는 제37항에 따른 조성물.
- 샤르코-마리-투스 2A(CMT2A) 질환 또는 신경병증을 갖는 환자의 치료를 위한 약제를 제조하는데 사용하기 위한 제1항 내지 제12항에 따른 재조합 AAV, 제13항 내지 제36항 중 어느 한 항에 따른 벡터, 또는 제37항에 따른 조성물.
- 하기로부터 선택되는 하나 이상의 공동-요법과 조합한 제39항 또는 제40항에 따른 환자를 치료하는 방법 또는 제41항 또는 제42항에 따른 벡터의 용도: 아세트아미노펜, 비스테로이드성 항염증 약물(NSAID), 삼환계 항우울제 또는 항간질 약물, 예컨대 카르바마제핀 또는 가바펜틴.
- 하기를 공동-투여하는 것을 포함하는, CMT2A를 갖는 환자를 치료하기 위한 병용 요법:
(a) 조작된 인간 미토푸신 2 (hMfn2) 암호화 서열을 포함하는 재조합 핵산 서열로서, 조작된 인간 미토푸신 2 (hMfn2) 암호화 서열은 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되며, 상기 조작된 hMfn2 암호화 서열은 서열번호 11의 서열 또는 이와 적어도 95% 동일한 서열을 갖고, (b)의 miRNA 표적 부위에 미스매치를 가짐으로써 CMT2A 환자의 내인성 인간 미토푸신 2 암호화 서열과 상이한, 재조합 핵산 서열,
(b) 인간 CMT2A 대상체의 내인성 hMfn2 암호화 서열에 특이적인 miRNA에 대한 적어도 하나의 암호화 서열을 포함하는 핵산으로서, 상기 miRNA 암호화 서열은 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되고, 상기 miRNA는 (a)의 조작된 hMfn2 암호화 서열 또는 이의 암호화된 mRNA에 결합하지 않는, 핵산. - 제44항에 있어서, 상기 miRNA 암호화 서열은 서열번호 89 또는 서열번호 89와 적어도 99% 동일한 것을 포함하는, 병용 요법.
- 하기를 공동-투여하는 것을 포함하는, CMT2A를 갖는 환자를 치료하기 위한 병용 요법:
(a) 조작된 인간 미토푸신 2(hMfn2) 암호화 서열을 포함하는 재조합 핵산 서열로서, 조작된 인간 미토푸신 2(hMfn2) 암호화 서열은 인간 표적 세포에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되며, 상기 조작된 hMfn2 암호화 서열은 (b))의 서열 중 miRNA 표적 부위에 미스매치를 가짐으로써 CMT2A 환자의 내인성 인간 미토푸신 2와 상이하도록 조작된 것인, 재조합 핵산 서열,
(b) 인간 CMT2A 대상체의 내인성 인간 미토푸신 2 암호화 서열에 특이적인 miRNA를 포함하는 적어도 하나의 핵산 서열로서, 상기 miRNA 암호화 서열은 대상체에서 이의 발현을 지시하는 조절 서열에 작동가능하게 연결되고, 상기 적어도 하나의 miRNA는 서열번호 15 (miR1693, 64 nt)를 포함하는 miRNA 암호화 서열; 서열번호 15의 적어도 60개의 연속적인 뉴클레오타이드를 포함하는 miRNA 암호화 서열; 서열번호 15와 적어도 99% 동일성을 포함하는 miRNA 암호화 서열로서, 이는 서열번호 15 (또는 서열번호 68)의 약 6개의 뉴클레오타이드 내지 약 26개의 뉴클레오타이드와 100% 동일성을 갖는 서열을 포함하는, miRNA 암호화 서열; 또는
(i) TTGACGTCCAGAACCTGTTCT, 서열번호 27;
(ii) AGAAGTGGGCACTTAGAGTTG, 서열번호 28;
(iii) TTCAGAAGTGGGCACTTAGAG, 서열번호 29;
(iv) TTGTCAATCCAGCTGTCCAGC, 서열번호 30;
(v) CAAACTTGGTCTTCACTGCAG, 서열번호 31;
(vi) AAACCTTGAGGACTACTGGAG, 서열번호 32;
(vii) TAACCATGGAAACCATGAACT, 서열번호 33;
(viii) ACAACAAGAATGCCCATGGAG, 서열번호 34;
(ix) AAAGGTCCCAGACAGTTCCTG, 서열번호 35;
(x) TGTTCATGGCGGCAATTTCCT, 서열번호 36;
(xi) TGAGGTTGGCTATTGATTGAC, 서열번호 37;
(xii) TTCTCACACAGTCAACACCTT, 서열번호 38;
(xiii) TTTCCTCGCAGTAAACCTGCT, 서열번호 39;
(xiv) AGAAATGGAACTCAATGTCTT, 서열번호 40;
(xiv) TGAACAGGACATCACCTGTGA, 서열번호 41;
(xvi) AATACAAGCAGGTATGTGAAC, 서열번호 42;
(xvii) TAAACCTGCTGCTCCCGAGCC, 서열번호 43;
(xviii) TAGAGGAGGCCATAGAGCCCA, 서열번호 44;
(xix) TCTACCCGCAGGAAGCAATTG, 서열번호 45; 또는
(xx) CTCCTTAGCAGACACAAAGAA, 서열번호 46, 또는 (i) 내지 (xx) 중 임의의 조합 중 하나 이상을 포함하는 miRNA 암호화 서열 중 하나 이상의 서열을 갖는, 적어도 하나의 miRNA. - 제44항 내지 제46항 중 어느 한 항에 있어서, 상기 제1 벡터는 핵산 (a)를 포함하고, 제2의 상이한 벡터는 적어도 하나의 miRNA (b)를 포함하는, 병용 요법.
- 제47항에 있어서, 상기 제1 벡터는 바이러스 벡터이고/이거나, 제2 벡터는 바이러스 벡터이고, 제1 및 제2 바이러스 벡터는 동일한 바이러스 공급원 유래일 수 있거나 상이할 수 있는, 병용 요법.
- 제47항 또는 제48항에 있어서, 상기 제1 벡터는 비-바이러스 벡터이고, 제2 벡터는 비-바이러스 벡터이고, 제1 및 제2 벡터는 동일한 조성물일 수 있거나 상이할 수 있는, 병용 요법.
Applications Claiming Priority (5)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| US202063051336P | 2020-07-13 | 2020-07-13 | |
| US63/051,336 | 2020-07-13 | ||
| US202163173045P | 2021-04-09 | 2021-04-09 | |
| US63/173,045 | 2021-04-09 | ||
| PCT/US2021/041406 WO2022015715A1 (en) | 2020-07-13 | 2021-07-13 | Compositions useful for treatment of charcot-marie-tooth disease |
Publications (1)
| Publication Number | Publication Date |
|---|---|
| KR20230038503A true KR20230038503A (ko) | 2023-03-20 |
Family
ID=77317406
Family Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| KR1020237003861A KR20230038503A (ko) | 2020-07-13 | 2021-07-13 | 샤르코-마리-투스 질환의 치료에 유용한 조성물 |
Country Status (14)
| Country | Link |
|---|---|
| US (1) | US20230270884A1 (ko) |
| EP (1) | EP4179097A1 (ko) |
| JP (1) | JP2023534037A (ko) |
| KR (1) | KR20230038503A (ko) |
| CN (1) | CN116438311A (ko) |
| AU (1) | AU2021309645A1 (ko) |
| BR (1) | BR112023000578A2 (ko) |
| CA (1) | CA3185281A1 (ko) |
| CO (1) | CO2023001500A2 (ko) |
| IL (1) | IL299762A (ko) |
| MX (1) | MX2023000658A (ko) |
| TW (1) | TW202216244A (ko) |
| WO (1) | WO2022015715A1 (ko) |
| ZA (1) | ZA202300505B (ko) |
Family Cites Families (25)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| US6759237B1 (en) | 1998-11-05 | 2004-07-06 | The Trustees Of The University Of Pennsylvania | Adeno-associated virus serotype 1 nucleic acid sequences, vectors and host cells containing same |
| CN103555678B (zh) | 2001-11-13 | 2018-02-09 | 宾夕法尼亚大学托管会 | 检测和/或鉴定腺伴随病毒(aav)序列以及分离所鉴定的新型序列的方法 |
| EP2359869B1 (en) | 2001-12-17 | 2018-12-26 | The Trustees Of The University Of Pennsylvania | Adeno-associated virus (AAV) serotype 8 sequences, vectors containing same and uses therefor |
| ES2874298T3 (es) | 2003-09-30 | 2021-11-04 | Univ Pennsylvania | Clados de virus adenoasociados (AAV), secuencias, vectores que contienen el mismo, y usos de los mismos |
| DK2359867T3 (en) | 2005-04-07 | 2015-01-05 | Univ Pennsylvania | A method for increasing an AAV vector function |
| EP2007795B1 (en) | 2006-03-30 | 2016-11-16 | The Board Of Trustees Of The Leland Stanford Junior University | Aav capsid proteins |
| AU2009311667B2 (en) | 2008-11-07 | 2016-04-14 | Massachusetts Institute Of Technology | Aminoalcohol lipidoids and uses thereof |
| SG10201908848RA (en) | 2010-03-29 | 2019-10-30 | Univ Pennsylvania | Pharmacologically induced transgene ablation system |
| US20130037977A1 (en) | 2010-04-08 | 2013-02-14 | Paul A. Burke | Preparation of Lipid Nanoparticles |
| US8853377B2 (en) | 2010-11-30 | 2014-10-07 | Shire Human Genetic Therapies, Inc. | mRNA for use in treatment of human genetic diseases |
| EP4043025A1 (en) | 2011-06-08 | 2022-08-17 | Translate Bio, Inc. | Lipid nanoparticle compositions and methods for mrna delivery |
| FR2977562B1 (fr) | 2011-07-06 | 2016-12-23 | Gaztransport Et Technigaz | Cuve etanche et thermiquement isolante integree dans une structure porteuse |
| US20150126589A1 (en) | 2012-06-08 | 2015-05-07 | Ethris Gmbh | Pulmonary Delivery of Messenger RNA |
| EP2929035A1 (en) | 2012-12-07 | 2015-10-14 | Shire Human Genetic Therapies, Inc. | Lipidic nanoparticles for mrna delivering |
| WO2015074085A1 (en) | 2013-11-18 | 2015-05-21 | Arcturus Therapeutics, Inc. | Ionizable cationic lipid for rna delivery |
| US11015174B2 (en) | 2015-12-11 | 2021-05-25 | The Trustees Of The University Of Pennsylvania | Scalable purification method for AAV8 |
| US11015173B2 (en) | 2015-12-11 | 2021-05-25 | The Trustees Of The University Of Pennsylvania | Scalable purification method for AAV1 |
| WO2017160360A2 (en) | 2015-12-11 | 2017-09-21 | The Trustees Of The University Of Pennsylvania | Scalable purification method for aav9 |
| WO2017100704A1 (en) | 2015-12-11 | 2017-06-15 | The Trustees Of The University Of Pennsylvania | Scalable purification method for aavrh10 |
| FI3589730T3 (fi) | 2017-02-28 | 2024-02-22 | Univ Pennsylvania | Kladin f adenoassosioitunut virus (aav) -vektori ja sen käyttötapoja |
| WO2018168961A1 (ja) | 2017-03-16 | 2018-09-20 | 株式会社デンソー | 自己位置推定装置 |
| AU2019228504A1 (en) | 2018-02-27 | 2020-09-10 | The Trustees Of The University Of Pennsylvania | Novel adeno-associated virus (AAV) vectors, AAV vectors having reduced capsid deamidation and uses therefor |
| AU2019227726A1 (en) | 2018-02-27 | 2020-09-10 | The Trustees Of The University Of Pennsylvania | Novel adeno-associated virus (AAV) vectors, aav vectors having reduced capsid deamidation and uses therefor |
| EP3844284A1 (en) * | 2018-08-29 | 2021-07-07 | Research Institute at Nationwide Children's Hospital | Products and methods for inhibition of expression of mutant gars protein |
| WO2020132455A1 (en) | 2018-12-21 | 2020-06-25 | The Trustees Of The University Of Pennsylvania | Compositions for drg-specific reduction of transgene expression |
-
2021
- 2021-07-13 EP EP21754870.0A patent/EP4179097A1/en active Pending
- 2021-07-13 JP JP2023502675A patent/JP2023534037A/ja active Pending
- 2021-07-13 WO PCT/US2021/041406 patent/WO2022015715A1/en active Application Filing
- 2021-07-13 KR KR1020237003861A patent/KR20230038503A/ko unknown
- 2021-07-13 AU AU2021309645A patent/AU2021309645A1/en active Pending
- 2021-07-13 MX MX2023000658A patent/MX2023000658A/es unknown
- 2021-07-13 IL IL299762A patent/IL299762A/en unknown
- 2021-07-13 US US18/005,504 patent/US20230270884A1/en active Pending
- 2021-07-13 TW TW110125641A patent/TW202216244A/zh unknown
- 2021-07-13 CN CN202180062652.6A patent/CN116438311A/zh active Pending
- 2021-07-13 CA CA3185281A patent/CA3185281A1/en active Pending
- 2021-07-13 BR BR112023000578A patent/BR112023000578A2/pt unknown
-
2023
- 2023-01-11 ZA ZA2023/00505A patent/ZA202300505B/en unknown
- 2023-02-10 CO CONC2023/0001500A patent/CO2023001500A2/es unknown
Also Published As
| Publication number | Publication date |
|---|---|
| CO2023001500A2 (es) | 2023-05-19 |
| AU2021309645A1 (en) | 2023-02-09 |
| ZA202300505B (en) | 2023-09-27 |
| CN116438311A (zh) | 2023-07-14 |
| MX2023000658A (es) | 2023-02-23 |
| TW202216244A (zh) | 2022-05-01 |
| JP2023534037A (ja) | 2023-08-07 |
| CA3185281A1 (en) | 2022-01-20 |
| EP4179097A1 (en) | 2023-05-17 |
| US20230270884A1 (en) | 2023-08-31 |
| WO2022015715A1 (en) | 2022-01-20 |
| BR112023000578A2 (pt) | 2023-05-09 |
| IL299762A (en) | 2023-03-01 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| KR20180008641A (ko) | 심부 인트론 돌연변이의 유전자 편집 | |
| JP2016517278A (ja) | スタッファー/フィラーポリヌクレオチド配列を含むベクターおよびその使用方法 | |
| RU2764919C2 (ru) | Оптимизированные гены и экспрессионные кассеты cln1, и их применение | |
| CN111356763B (zh) | 变体RNAi | |
| AU2018248304C1 (en) | Minigene therapy | |
| KR20220133854A (ko) | 유전적 청력 상실 치료를 위한 아데노 관련 바이러스(aav) 시스템 | |
| KR20200104307A (ko) | 뮤코다당류증 iiia형에 대한 유전자 요법 | |
| CN113710281A (zh) | 用于治疗grn相关成人发作性神经退行性病变的重组腺相关病毒 | |
| KR20220105158A (ko) | 이식유전자 발현의 drg-특이적 감소를 위한 조성물 | |
| CN115029360A (zh) | 用于治疗粘多糖贮积症iiia型的转基因表达盒 | |
| CN116685329A (zh) | 核酸构建体及其用于治疗脊髓性肌肉萎缩症的用途 | |
| CN114127296A (zh) | Ube3a基因和表达盒及其应用 | |
| CA3098592A1 (en) | Gene therapy for treating peroxisomal disorders | |
| KR20220145838A (ko) | Gm1 강글리오사이드증을 치료하는 데 유용한 조성물 | |
| KR20230038503A (ko) | 샤르코-마리-투스 질환의 치료에 유용한 조성물 | |
| KR20230117731A (ko) | 청력 상실의 치료를 위한 변이체 아데노-연관된 바이러스(aav) 캡시드 폴리펩티드 및 이의 유전자 치료제 | |
| KR20210132095A (ko) | 크라베병의 치료에 유용한 조성물 | |
| WO2023049846A1 (en) | Compositions useful for treatment of charcot-marie-tooth disease | |
| US20240033375A1 (en) | Compositions useful for treating spinal and bulbar muscular atrophy (sbma) | |
| JP2024515612A (ja) | 球脊髄性筋萎縮症(sbma)の治療に有用な組成物 | |
| TW202340467A (zh) | 有用於治療c9orf72介導之病症之組成物及方法 | |
| CN116057175A (zh) | 可用于治疗克拉伯病的组合物 | |
| CN116209430A (zh) | 囊泡靶向蛋白及其用途 | |
| CN116670159A (zh) | 组合物及其用于治疗安格尔曼综合征的用途 | |
| WO2022147490A1 (en) | Optimized fukutin-related proteins (fkrp) and methods of use |