KR20220139924A - 큰 유전자 벡터 및 그의 전달 및 용도 - Google Patents
큰 유전자 벡터 및 그의 전달 및 용도 Download PDFInfo
- Publication number
- KR20220139924A KR20220139924A KR1020227030657A KR20227030657A KR20220139924A KR 20220139924 A KR20220139924 A KR 20220139924A KR 1020227030657 A KR1020227030657 A KR 1020227030657A KR 20227030657 A KR20227030657 A KR 20227030657A KR 20220139924 A KR20220139924 A KR 20220139924A
- Authority
- KR
- South Korea
- Prior art keywords
- sequence
- seq
- protein
- leu
- strc
- Prior art date
Links
Images
Classifications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/63—Introduction of foreign genetic material using vectors; Vectors; Use of hosts therefor; Regulation of expression
- C12N15/79—Vectors or expression systems specially adapted for eukaryotic hosts
- C12N15/85—Vectors or expression systems specially adapted for eukaryotic hosts for animal cells
- C12N15/86—Viral vectors
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K48/00—Medicinal preparations containing genetic material which is inserted into cells of the living body to treat genetic diseases; Gene therapy
- A61K48/005—Medicinal preparations containing genetic material which is inserted into cells of the living body to treat genetic diseases; Gene therapy characterised by an aspect of the 'active' part of the composition delivered, i.e. the nucleic acid delivered
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K48/00—Medicinal preparations containing genetic material which is inserted into cells of the living body to treat genetic diseases; Gene therapy
- A61K48/0075—Medicinal preparations containing genetic material which is inserted into cells of the living body to treat genetic diseases; Gene therapy characterised by an aspect of the delivery route, e.g. oral, subcutaneous
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61P—SPECIFIC THERAPEUTIC ACTIVITY OF CHEMICAL COMPOUNDS OR MEDICINAL PREPARATIONS
- A61P27/00—Drugs for disorders of the senses
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61P—SPECIFIC THERAPEUTIC ACTIVITY OF CHEMICAL COMPOUNDS OR MEDICINAL PREPARATIONS
- A61P27/00—Drugs for disorders of the senses
- A61P27/16—Otologicals
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K14/00—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof
- C07K14/005—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof from viruses
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K14/00—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof
- C07K14/435—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof from animals; from humans
- C07K14/46—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof from animals; from humans from vertebrates
- C07K14/47—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof from animals; from humans from vertebrates from mammals
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/11—DNA or RNA fragments; Modified forms thereof; Non-coding nucleic acids having a biological activity
- C12N15/62—DNA sequences coding for fusion proteins
- C12N15/625—DNA sequences coding for fusion proteins containing a sequence coding for a signal sequence
-
- A—HUMAN NECESSITIES
- A01—AGRICULTURE; FORESTRY; ANIMAL HUSBANDRY; HUNTING; TRAPPING; FISHING
- A01K—ANIMAL HUSBANDRY; CARE OF BIRDS, FISHES, INSECTS; FISHING; REARING OR BREEDING ANIMALS, NOT OTHERWISE PROVIDED FOR; NEW BREEDS OF ANIMALS
- A01K2217/00—Genetically modified animals
- A01K2217/07—Animals genetically altered by homologous recombination
- A01K2217/075—Animals genetically altered by homologous recombination inducing loss of function, i.e. knock out
-
- A—HUMAN NECESSITIES
- A01—AGRICULTURE; FORESTRY; ANIMAL HUSBANDRY; HUNTING; TRAPPING; FISHING
- A01K—ANIMAL HUSBANDRY; CARE OF BIRDS, FISHES, INSECTS; FISHING; REARING OR BREEDING ANIMALS, NOT OTHERWISE PROVIDED FOR; NEW BREEDS OF ANIMALS
- A01K2227/00—Animals characterised by species
- A01K2227/10—Mammal
- A01K2227/105—Murine
-
- A—HUMAN NECESSITIES
- A01—AGRICULTURE; FORESTRY; ANIMAL HUSBANDRY; HUNTING; TRAPPING; FISHING
- A01K—ANIMAL HUSBANDRY; CARE OF BIRDS, FISHES, INSECTS; FISHING; REARING OR BREEDING ANIMALS, NOT OTHERWISE PROVIDED FOR; NEW BREEDS OF ANIMALS
- A01K2267/00—Animals characterised by purpose
- A01K2267/03—Animal model, e.g. for test or diseases
- A01K2267/0306—Animal model for genetic diseases
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K38/00—Medicinal preparations containing peptides
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K2319/00—Fusion polypeptide
- C07K2319/90—Fusion polypeptide containing a motif for post-translational modification
- C07K2319/92—Fusion polypeptide containing a motif for post-translational modification containing an intein ("protein splicing")domain
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2740/00—Reverse transcribing RNA viruses
- C12N2740/00011—Details
- C12N2740/10011—Retroviridae
- C12N2740/15011—Lentivirus, not HIV, e.g. FIV, SIV
- C12N2740/15041—Use of virus, viral particle or viral elements as a vector
- C12N2740/15043—Use of virus, viral particle or viral elements as a vector viral genome or elements thereof as genetic vector
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2750/00—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA ssDNA viruses
- C12N2750/00011—Details
- C12N2750/14011—Parvoviridae
- C12N2750/14111—Dependovirus, e.g. adenoassociated viruses
- C12N2750/14141—Use of virus, viral particle or viral elements as a vector
- C12N2750/14143—Use of virus, viral particle or viral elements as a vector viral genome or elements thereof as genetic vector
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2800/00—Nucleic acids vectors
- C12N2800/40—Systems of functionally co-operating vectors
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2830/00—Vector systems having a special element relevant for transcription
- C12N2830/50—Vector systems having a special element relevant for transcription regulating RNA stability, not being an intron, e.g. poly A signal
Abstract
본 개시내용은 이중-벡터 인테인-매개 단백질 트랜스-스플라이싱 시스템, 세포, 조성물 및 유전자 요법을 위한 그의 사용 방법을 제공한다. 일부 실시양태에서, 본 개시내용은 본원에 기재된 이중-벡터 시스템을 사용하여 STRC 단백질을 코딩하는 STRC 유전자를 전달함으로써 상염색체 열성 유형의 비-증후군성 난청인 DFNB16을 치료하기 위한 방법 및 조성물을 제공한다.
Description
관련 출원에 대한 상호-참조
본 PCT 국제 출원은 2020년 2월 7일에 출원된 미국 가출원 번호 62/971,555를 우선권 주장하며, 이는 모든 목적을 위해 그 전문이 본원에 참조로 포함된다.
청력 상실은 선진국 또는 산업화 국가에서 가장 흔한 신경계 장애 중 하나이고, 전세계적으로 4억 6천 6백만건 초과의 사례를 차지하는 가장 보편적인 감각신경성 장애이다. 비-증후군성 난청 또는 비-증후군성 유전적 난청은 임의의 다른 징후 또는 증상과 연관되지 않은 청력 상실이다. 4가지 유형의 비-증후군성 난청이 있다: DFNA (상염색체 우성), DFNB (상염색체 열성), DFNX (X-연관) 및 미토콘드리아 비-증후군성 난청. 비-증후군성 난청 중 16번째로 기재된 상염색체 열성 유형인 DFNB16은 스테레오실린으로 공지된 세포외 구조 단백질을 코딩하는 STRC 유전자 내의 돌연변이에 의해 유발된 단일유전자, 비-증후군성, 열성 청력 상실이다. 내이에서의 STRC의 정상 발현은 청각 기능에 필수적이다. 내이 내 감각 유모 세포의 정점에 있는 변형된 미세융모의 상단에서 발견되는 스테레오실린은 내이 내 특수 세포로부터 돌출된, 부동섬모로 공지된 유모-유사 구조와 회합된다. STRC 내의 돌연변이는 중등도 내지 중증 청력 상실을 유발하고, 미국에서 추정컨대 ~50,000명의 환자에 영향을 미치며, 따라서 유전자 요법을 위한 매력적인 후보이다. 스테레오실린은 응집성 미세융모 다발을 유지하고, 다발을 내이의 와우 내에 있는 위에 놓인 덮개막에 커플링시키는 기능을 한다. 전세계적 통계는 DFNB16이, 특히 중등도 청력 장애를 갖는 대상체에서 유전적 난청의 유의한 비율을 구성한다는 것을 시사한다. 파트너스 래보러토리 오브 몰레큘라 메디신(Partners Laboratory of Molecular Medicine)으로부터의 데이터에 기초하면, 보스턴에서 시험된 유전적 청력 상실 환자의 19%는 STRC에 돌연변이를 가지며, 이에 따라 그것은 유전적 청력 상실의 두번째로 가장 흔한 형태이고, 내이의 감각 유모 세포에 영향을 미치는 가장 흔한 형태이다. 약 40개의 상이한 돌연변이 (주로 열성)가 STRC 유전자에서 확인되었으며, 대다수는 결함성 스테레오실린의 합성을 유도하거나 또는 그의 합성을 완전히 방지한다. 정상 STRC 단백질의 결여는 적절한 소리 유발 자극에 요구되는 위에 놓인 덮개막으로부터 감각 유모 다발을 탈커플링시킨다. DFNB16 환자는 중등도 내지 중증 청력 상실을 갖고, 전형적으로 보청기 또는 와우 이식물로 치료된다. 그러나, 현재 DFNB16 청력 상실에 대한 생물학적 치료는 없다.
AAV는 유전성 장애의 유전자 요법 치료를 위한 매력적인 벡터 시스템을 제공한다. 안전성 관점에서 이들 및 유전자 전달. 재조합 AAV (rAAV)는 비-병원성 및 복제-결함성 바이러스로부터 유래되고, 그의 숙주 세포에 대해 비-세포독성이다. 더욱이, rAAV는 또 다른 안전성 특색을 제시하는 역전된 말단 반복부 (ITR)를 제외하고 모든 바이러스 DNA 서열이 결여되어 있다. ITR은 AAV DNA 복제, 패키징, 염색체 통합 및 프로-바이러스 구출에 필요하다. AAV 벡터는 또한 효과적인 트랜스진 전달 및 예를 들어 내이 세포에서의 지속적인 발현을 위한 강력한 도구인 것으로 입증되었다. 그러나, 내이 기능에 중요한 많은 단백질은 STRC의 적재 용량 (~5.8 kB)을 비롯하여 AAV 벡터의 적재 용량 (~4.5 kB)을 초과하는 코딩 서열을 갖는다. 따라서, 상기 언급된 임의의 유전자 요법, 구축물 및 벡터의 효과적인 형태로서 큰 유전자 (예를 들어, 4 kB 초과)에 의해 코딩되는 단백질의 전달 및 발현 방법이 필요하다.
따라서, 본 개시내용의 목적은 유전자 돌연변이를 앓고 있는 대상체를 치료하기 위한 큰 유전자 (예를 들어, 4 kB 초과)에 대한 유전자 요법을 제공하는 것이다. 유전자 요법은, 예를 들어 DFNB16 청력 상실을 갖는 소아 및 성인에서 청력의 예방 및/또는 회복을 가능하게 할 수 있다.
또 다른 목적은 큰 유전자 서열 (예를 들어, 4 kB 초과; STRC)을 전달하는 방법 및 큰 유전자 서열을 전달하기 위한 벡터 및 구축물을 제공하는 것이며, 여기서 방법은 벡터 크기 한계를 극복한다.
한 측면은
a) 5'에서 3' 방향으로:
- 관심 단백질의 아미노 말단 (N-말단) 부분을 코딩하는 부분 코딩 서열의 5'-말단에 있는 신호 서열 (예를 들어, 서열식별번호: 9; 서열식별번호: 11);
- 관심 단백질의 N-말단 부분 (예를 들어, N-STRC; 서열식별번호: 15; 서열식별번호: 16)을 코딩하는 부분 코딩 서열;
- 부분 코딩 서열에 인접하고 그의 하류인 스플라이스 공여자 서열을 코딩하는 서열 (예를 들어, 인테인의 N-말단 단편 (N-인테인), 또한 스플릿 인테인-N으로도 공지됨; 서열식별번호: 14를 코딩하는 서열식별번호: 13)
을 포함하는 제1 뉴클레오티드 서열 (예를 들어, 서열식별번호: 5; 서열식별번호: 7)을 포함하는 제1 벡터; 및
b) 5'에서 3' 방향으로:
- 관심 단백질의 카르복시 말단 (C-말단) 부분을 코딩하는 부분 코딩 서열의 5'-말단에 있는 신호 서열 (예를 들어, 서열식별번호: 9; 서열식별번호: 11);
- 신호 서열 및 관심 단백질의 C-말단 부분을 코딩하는 부분 코딩 서열이 플랭킹된 스플라이스 수용자 서열을 코딩하는 서열 (예를 들어, 인테인의 C-말단 단편 (C-인테인), 또한 스플릿 인테인-C로도 공지됨; 서열식별번호: 22를 코딩하는 서열식별번호: 21);
- 관심 단백질의 C-말단 부분 (예를 들어, C-STRC; 서열식별번호: 23; 서열식별번호: 24)을 코딩하는 부분 코딩 서열
을 포함하는 제2 뉴클레오티드 서열 (예를 들어, 서열식별번호: 17; 서열식별번호: 19)을 포함하는 제2 벡터
를 포함하는, 세포에서 관심 단백질을 발현시키기 위한 벡터 시스템 (예를 들어, 이중-벡터 시스템)을 제공한다.
또 다른 측면은
a) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 관심 단백질의 아미노 말단 (N-말단) 부분 (예를 들어, N-STRC)을 코딩하는 부분 코딩 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 인테인의 아미노 말단 단편 (N-인테인)을 코딩하는 서열;
- 폴리-아데닐화 (폴리A) 신호 서열;
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터; 및
b) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 인테인의 카르복시 말단 단편 (C-인테인)을 코딩하는 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 관심 단백질의 카르복시 말단 (C-말단) 부분 (예를 들어, C-STRC)을 코딩하는 부분 코딩 서열;
- 폴리-아데닐화 (폴리A) 신호 서열;
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제2 뉴클레오티드 서열을 포함하는 제2 벡터
를 포함하는, 세포에서 관심 단백질을 발현하기 위한 이중-벡터 시스템을 제공한다.
이중-벡터 시스템의 또 다른 측면은 세포에서 제1 벡터 및 제2 벡터가 각각
a) N-말단에서 C-말단 방향으로:
- 신호 펩티드 서열, 이에 연결된 관심 단백질 (예를 들어, STRC) 서열의 N-말단 부분, 이의 C-말단 단부에서 융합된 N-인테인 단백질 서열
을 포함하는 제1 단백질 서열; 및
b) N-말단에서 C-말단 방향으로:
- 신호 펩티드 서열, 이에 연결된 C-인테인 단백질 서열, 이에 N-말단 단부가 융합된 관심 단백질 (예를 들어, STRC) 서열의 C-말단 부분
을 포함하는 제2 단백질 서열
을 발현하는 것을 제공한다.
또 다른 측면은 관심 단백질의 N-말단 부분 (예를 들어, N-STRC) 및 관심 단백질의 C-말단 부분 (예를 들어, C-STRC)이 전장 관심 단백질 (예를 들어, STRC)을 형성하는 것을 제공한다. 일부 측면에서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열은 동일하거나 상이하거나 또는 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열은 제1 단백질 서열 및 제2 단백질 서열을 동일한 세포 구획으로 수송하도록 구성된다. 추가 측면은 서열식별번호: 9 또는 서열식별번호: 11에 대해 적어도 80% 동일성을 갖는 핵산 서열을 포함하고 서열식별번호: 10 또는 서열식별번호: 12에 대해 적어도 80% 동일성을 갖는 아미노산 서열을 갖는 신호 펩티드 서열을 코딩하는 신호 서열에 관한 것일 수 있다. 다른 측면은 아데노-연관 바이러스 (AAV) 벡터 또는 렌티바이러스일 수 있는 바이러스 벡터일 수 있는 벡터 (예를 들어, 제1 벡터 및 제2 벡터)를 제공한다. 한 측면은 동일하거나 상이한 혈청형을 갖는 바이러스 벡터에 관한 것일 수 있다. 이중-벡터 시스템의 또 다른 측면은 관심 단백질의 인테인-매개 트랜스-스플라이싱을 제공하며, 여기서 관심 단백질의 N-말단 부분 (예를 들어, N-STRC) 및 관심 단백질의 C-말단 부분 (예를 들어, C-STRC)은 펩티드 결합을 통해 전장 관심 단백질 (예를 들어, STRC)을 형성할 수 있고, 여기서 관심 단백질은 STRC 유전자에 의해 코딩되는 STRC 단백질일 수 있다. 관심 단백질의 N-말단 부분 (예를 들어, N-STRC; 인간 서열식별번호: 15 또는 뮤린 서열식별번호: 16)을 코딩하는 뉴클레오티드 서열은, 전장 관심 단백질 (예를 들어, STRC; 서열식별번호: 25 또는 서열식별번호: 26)의 N-말단 부분의 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 또는 그의 54% 미만 (예를 들어, 53%, 52%, 51%, 50%, 45%, 43%, 41%) 및/또는 그에 대해 54% 미만의 동일성 및/또는 그의 54% 미만의 길이의 관심 아미노산 서열 (예를 들어, STRC; 서열식별번호: 6; 서열식별번호: 8; 서열식별번호: 15 또는 서열식별번호: 16)을 코딩하는, 관심 뉴클레오티드 서열 (예를 들어, STRC; 서열식별번호: 5 또는 서열식별번호: 7)에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함한다. 또 다른 측면은 전장 관심 단백질 (예를 들어, 서열식별번호: 25 또는 서열식별번호: 26)의 N-말단 부분의 41% 이상 (예를 들어, 42%, 43%, 44%, 45%, 50%, 51%, 52%, 53%) 및/또는 그에 대해 41% 이상의 동일성 및/또는 그의 41% 이상의 길이의 아미노산 서열을 포함하는 관심 단백질 (예를 들어, STRC)의 N-말단 부분을 제공한다.
추가 측면은 목적하는 신호 펩티드 서열 (예를 들어, 서열식별번호: 10; 서열식별번호: 12)에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 갖는 신호 펩티드 서열을 코딩하는, 목적하는 신호 서열 (예를 들어, 서열식별번호: 9; 서열식별번호: 11)에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 갖는 신호 서열을 포함하는 뉴클레오티드 서열을 제공한다.
또 다른 측면은 목적하는 N-인테인 아미노산 서열 (예를 들어, 서열식별번호: 14)에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 목적하는 N-인테인 아미노산 서열을 코딩하는, 목적하는 N-인테인 뉴클레오티드 서열 (예를 들어, 서열식별번호: 13)에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함하는 목적하는 N-인테인 서열을 제공할 수 있다. 추가 측면은 목적하는 C-인테인 아미노산 서열 (예를 들어, 서열식별번호: 22)에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 목적하는 C-인테인 아미노산 서열을 코딩하는, 목적하는 C-인테인 뉴클레오티드 서열 (예를 들어, 서열식별번호: 21)에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함하는 목적하는 C-인테인 서열에 관한 것일 수 있다.
본 개시내용의 이중-벡터 시스템의 또 다른 측면에서, 관심 단백질 (예를 들어, STRC)의 C-말단 부분은, 전장 관심 단백질 (예를 들어, STRC; 서열식별번호: 25; 서열식별번호: 26)의 C-말단 부분의 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 또는 그의 46% 이상 및/또는 그에 대해 46% 이상의 동일성 및/또는 그의 46% 이상의 길이의 관심 아미노산 서열 (예를 들어, STRC; 서열식별번호: 18; 서열식별번호: 20; 서열식별번호: 23; 서열식별번호: 24)을 코딩하는, 뉴클레오티드 서열 (예를 들어, STRC; 서열식별번호: 17; 서열식별번호: 19)에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함할 수 있다. 또 다른 측면은 전장 관심 단백질 (예를 들어, STRC; 서열식별번호: 25; 서열식별번호: 26)의 C-말단 부분에 대해 60% 이하의 동일성 및/또는 그의 60% 이하의 길이의 아미노산 서열을 포함하는 관심 단백질 (예를 들어, STRC)의 C-말단 부분을 제공할 수 있다.
추가 측면은 숙주 세포에서 STRC 유전자의 코딩 서열을 발현시키기 위한 벡터 시스템이며, 여기서 코딩 서열은, 예를 들어 인간 STRC: 서열식별번호: 1 또는 서열식별번호: 30 또는 뮤린 STRC: 서열식별번호: 3 또는 서열식별번호: 32의 STRC 뉴클레오티드 코딩 서열을 포함하는 적어도 1개의 벡터를 포함하고, 여기서 STRC 뉴클레오티드 코딩 서열은, 예를 들어 서열식별번호: 2 또는 서열식별번호: 25 또는 서열식별번호: 4 또는 서열식별번호: 26의 STRC 단백질을 코딩하는 것인 벡터 시스템을 제공할 수 있다. 또 다른 측면은 목적하는 전장 단백질을 코딩하는 뉴클레오티드 서열이며, 여기서 뉴클레오티드 서열은, 예를 들어 인간 STRC: 서열식별번호: 1 또는 서열식별번호: 33 또는 뮤린 STRC: 서열식별번호: 3 또는 서열식별번호: 39를 포함하고, 이는 목적하는 단백질, 예를 들어 인간 STRC: 서열식별번호: 2 또는 서열식별번호: 25 또는 뮤린 STRC: 서열식별번호: 4 또는 서열식별번호: 26을 코딩하는 것인 뉴클레오티드 서열에 관한 것일 수 있다.
벡터 시스템의 한 측면은 본원에 기재된 바와 같은 숙주 세포에서 STRC 유전자의 코딩 서열을 발현시키기 위한 이중-벡터 시스템을 포함하며, 여기서 이중-벡터 시스템은 목적하는 관심 핵산 서열 (예를 들어, 서열식별번호: 5; 서열식별번호: 7)에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 목적하는 핵산 서열을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터를 제공한다. 한 측면에서, 제1 벡터 (예를 들어, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈)는 5'에서 3' 방향으로: 부분 코딩 서열의 5'-말단에 있는 신호 서열 (예를 들어, 서열식별번호: 10을 코딩하는 서열식별번호: 9; 또는 서열식별번호: 12를 코딩하는 서열식별번호: 11); 관심 단백질 (예를 들어, STRC; 서열식별번호: 15; 서열식별번호: 16)의 아미노 말단 (N-말단) 부분을 코딩하는 부분 코딩 서열; 부분 코딩 서열에 플랭킹되거나 인접할 수 있는 스플라이스 공여자 서열을 코딩하는 하류 서열 (예를 들어, N-말단 인테인 (N-인테인, 또한 스플릿 인테인-N으로도 공지됨); 서열식별번호: 14를 코딩하는 서열식별번호: 13)을 포함하는 제1 뉴클레오티드 서열 (예를 들어, 서열식별번호: 6을 코딩하는 서열식별번호: 5; 서열식별번호: 8을 코딩하는 서열식별번호: 7)을 포함한다. 또 다른 측면은 관심 단백질의 N-말단 부분을 포함하고, 또한 신호 서열 및 목적하는 N-인테인 단백질을 코딩하는 서열, 뿐만 아니라 역전된 말단 반복부 (ITR), 프로모터 및 폴리-아데닐화 (폴리A) 서열을 함유하는 제1 뉴클레오티드 서열을 포함한다. 제1 뉴클레오티드 서열은 목적하는 아미노산 서열 (예를 들어, 서열식별번호: 5; 서열식별번호: 16) 또는 전장 관심 아미노산 서열 (예를 들어, 서열식별번호: 25; 서열식별번호: 26)에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 관심 아미노산 서열을 코딩할 수 있다.
본 개시내용의 이중-벡터 시스템의 또 다른 측면은 또한 목적하는 관심 핵산 서열 (예를 들어, 서열식별번호: 17; 서열식별번호: 19)에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 목적하는 핵산 서열의 나머지 부분을 포함하는 제2 뉴클레오티드 서열을 제공한다. 한 측면에서, 제2 벡터 (예를 들어, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈)는 5'에서 3' 방향으로: 신호 서열 (예를 들어, 서열식별번호: 10을 코딩하는 서열식별번호: 9; 또는 서열식별번호: 12를 코딩하는 서열식별번호: 11), 신호 서열이 그의 상류일 수 있는 스플라이스 수용자 서열 (예를 들어, C-말단 인테인 (C-인테인); 서열식별번호: 22를 코딩하는 서열식별번호: 21), 그에 바로 인접하여 위치하거나 플랭킹된 관심 단백질의 전장 코딩 서열의 나머지 부분, 즉 관심 단백질의 C-말단 부분 (예를 들어, STRC; 서열식별번호: 23; 서열식별번호: 24)을 코딩하는 하류 부분 코딩 서열을 포함하는 제2 뉴클레오티드 서열 (예를 들어, 서열식별번호: 18을 코딩하는 서열식별번호: 17; 서열식별번호: 20을 코딩하는 서열식별번호: 19)을 포함한다. 또 다른 측면은 관심 단백질의 C-말단 부분, 신호 서열을 코딩하는 서열 및 목적하는 C-인테인 단백질을 코딩하는 서열, 뿐만 아니라 역전된 말단 반복부 (ITR), 프로모터 및 폴리-아데닐화 (폴리A) 서열을 포함하는 제2 뉴클레오티드 서열을 포함한다. 일부 측면에서, 제2 뉴클레오티드 서열은 또한 링커 서열 및 myc 태그 서열을 함유할 수 있다. 제2 뉴클레오티드 서열은 목적하는 아미노산 서열 (예를 들어, 서열식별번호: 18; 서열식별번호: 20; 서열식별번호: 23; 서열식별번호: 24) 또는 전장 관심 아미노산 서열 (예를 들어, 서열식별번호: 25; 서열식별번호: 26)에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 코딩할 수 있다.
다른 측면은 목적하는 유전자 또는 그의 목적하는 단백질 (예를 들어, STRC 단백질)을 전달하기 위한 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템)을 함유하는 세포(들) 또는 숙주 세포(들)를 제공할 수 있다.
추가 측면은 목적하는 유전자 또는 그의 목적하는 단백질 (예를 들어, STRC 단백질)을 전달하기 위한 본 개시내용의 벡터 시스템 (예를 들어, 이중-벡터 시스템) 및 제약상 허용되는 비히클 (예를 들어, 희석제, 부형제)을 포함하는 제약 조성물에 관한 것일 수 있다.
또 다른 측면에서, 질환 또는 상태의 유전자 돌연변이를 앓고 있는, 그 질환 또는 상태의 치료를 필요로 하는 대상체에게 유효량의 본 개시내용의 벡터 시스템 (예를 들어, 이중-벡터 시스템)을 투여하는 것을 포함하는, 상기 대상체에서 질환 또는 상태를 치료하는 방법이며, 여기서 방법은 동일한 유전자 내의 유전자 돌연변이에 의해 유발된 질환 또는 상태를 앓고 있는 대상체에게 목적하는 야생형 또는 교정된 유전자 또는 목적하는 야생형 또는 교정된 단백질 (예를 들어, STRC)을 전달하여, 그에 의해 대상체에서 질환 또는 상태를 치료한다. 또 다른 측면은 상염색체 열성 청력 상실을 앓고 있는, 그 질환 또는 상태의 치료를 필요로 하는 대상체에게 목적하는 야생형 또는 교정된 유전자 또는 목적하는 야생형 또는 교정된 단백질 (예를 들어, STRC)을 전달하는 유효량의 본원에 기재된 이중-벡터 시스템을 투여하는 것을 포함하는, 상기 대상체에서 질환 또는 상태를 치료하는 방법을 제공한다. 상염색체 열성 청력 상실의 치료를 필요로 하는 대상체에게 목적하는 유전자 또는 그의 목적하는 단백질 (예를 들어, STRC 단백질)을 전달하기 위한 본원에 기재된 이중-벡터 시스템을 함유하는 세포(들) 또는 숙주 세포(들) 또는 제약 조성물 (제약상 허용되는 비히클 (예를 들어, 희석제, 부형제) 함유)을 투여하는 것을 포함하는, 대상체에서 상염색체 열성 청력 상실을 치료하는 방법을 제공한다. 또 다른 측면은 상염색체 열성 청력 상실, DFNB16을 제공할 수 있다.
한 측면에서, 본 개시내용의 방법은 대상체의 세포를 목적하는 유전자 또는 그의 목적하는 단백질 (예를 들어, STRC 단백질)을 전달하기 위한 본 개시내용의 벡터 시스템 (예를 들어, 이중-벡터 시스템) 및 제약상 허용되는 비히클 (예를 들어, 희석제, 부형제)을 포함하는 조성물과 접촉시키는 것을 포함할 수 있으며, 여기서 접촉은 제1 뉴클레오티드 서열 및 제2 뉴클레오티드 서열의 세포 내로의 전달을 일으키고, 여기서 세포는 펩티드 결합에 의해 연결된 목적하는 단백질의 N-말단 부분 및 목적하는 단백질의 C-말단 부분을 발현하여 전장의 목적하는 단백질을 형성할 수 있다. 또 다른 측면은 청력 상실을 특징으로 하는 병리상태 또는 질환의 치료 및/또는 예방을 필요로 하는 대상체에게 유효량의 본원에 기재된 이중-벡터 시스템을 투여하거나, 또는 목적하는 유전자 또는 그의 목적하는 단백질 (예를 들어, STRC 단백질)을 전달하기 위한 본원에 기재된 이중-벡터 시스템을 함유하는 세포 또는 제약 조성물 (제약상 허용되는 비히클 (예를 들어, 희석제, 부형제) 함유)을 투여하는 것을 포함하는, 청력 상실을 특징으로 하는 병리상태 또는 질환을 치료 및/또는 예방하는 방법을 제공한다. 일부 측면에서, 세포는 귀의 내이 세포, 내유모 세포 또는 외유모 세포일 수 있으며, 여기서 세포 또는 세포에의 투여 방법은 생체내, 생체외 및/또는 시험관내에서 이루어질 수 있다. 본 개시내용의 추가 측면은 본원에 기재된 임의의 방법이 대상체에서 청각 기능의 개선 또는 회복을 가져오는 것이다.
본 개시내용의 다른 특색 및 이점은 상세한 설명 및 청구범위로부터 분명할 것이다.
도 1은 AAV2 역전된 말단 반복부 (ITR), 프로모터 및 폴리-아데닐화 (폴리A) 서열을 갖는, 목적하는 전장 단백질 (예를 들어, STRC)의 발현을 위한 단일 벡터 시스템에 대한 구축물의 개략적 표현을 보여준다.
도 2a-2c는 인간 STRC 단백질을 코딩하는 뉴클레오티드 서열, 신호 펩티드 서열, 링커 서열, Myc 태그를 코딩하는 서열 및 출발 및 정지 코돈 (서열식별번호: 33)을 보여준다.
도 3은 도 2a-2c에 제시된 뉴클레오티드 서열에 의해 코딩되는 신호 펩티드 서열, 인간 STRC 단백질 서열, 링커 서열 및 myc 태그를 함유하는 아미노산 서열 (서열식별번호: 36)을 보여준다.
도 4a-4d는 뮤린 STRC 단백질을 코딩하는 뉴클레오티드 서열, 신호 펩티드 서열, 링커 서열, Myc 태그를 코딩하는 서열 및 출발 및 정지 코돈 (서열식별번호: 38)을 보여준다.
도 5는 도 4a 내지 4d에 제시된 뉴클레오티드 서열에 의해 코딩되는 신호 펩티드 서열, 뮤린 STRC 단백질 서열, 링커 서열 및 Myc 태그를 함유하는 아미노산 서열 (서열식별번호: 39)을 보여준다.
도 6은 AAV2 역전된 말단 반복부, 프로모터 및 폴리-아데닐화 서열을 사용한 이중 AAV 인테인-매개 스테레오실린 단백질 트랜스-스플라이싱의 개략적 표현을 보여준다. 인테인 단편은 단백질 재조합을 매개하고, 그 자체를 절제하고, 나머지 STRC 단편 (엑스테인)을 펩티드 결합으로 연결한다.
도 7a 및 7b는 인간 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 스플라이스 공여자 서열 (예를 들어, N-인테인; CFS-N-Strc-N-Int, 구축물 2, N-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 5)을 보여준다. 뉴클레오티드 서열은 신호 서열, 5' Strc (야생형 Strc 코딩 서열의 5' 단편) 및 N-인테인 서열 (인테인 단백질의 N-말단 단편을 코딩함)을 함유한다.
도 8a 및 8b는 뮤린 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 N-인테인 (예를 들어, CFS-N-Strc-N-Int, 구축물 2, N-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 7)을 보여준다. 뉴클레오티드 서열은 신호 서열, 5' Strc (야생형 Strc 코딩 서열의 5' 단편) 및 N-인테인 서열 (인테인 단백질의 N-말단 단편을 코딩함)을 함유한다.
도 9는 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱에 사용되는 신호 펩티드 서열, STRC 단백질의 N-말단 부분 및 N-인테인을 코딩하는 도 8a 및 8b의 뉴클레오티드 서열을 함유하는 구축물의 개략적 표현을 보여준다.
도 10은 도 7a 및 7b에 제시된 뉴클레오티드 서열에 의해 코딩되는 인간 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 N-인테인을 함유하는 아미노산 서열 (서열식별번호: 6)을 보여준다.
도 11은 도 8a 및 8b에 제시된 뉴클레오티드 서열에 의해 코딩되는 뮤린 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 N-인테인을 함유하는 아미노산 서열 (서열식별번호: 8)을 보여준다.
도 12a 및 12b는 인간 STRC 단백질의 C-말단 부분, 신호 펩티드 서열 및 C-인테인 (예를 들어, CFS-C-Strc-C-Int, 구축물 2, C-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 17)을 보여준다. 뉴클레오티드 서열은 신호 서열, C-인테인 서열 (인테인 단백질의 C-말단 단편을 코딩함), 3' Strc (야생형 Strc 코딩 서열의 3' 단편), 링커 서열 및 myc 태그 서열을 함유한다.
도 13a 및 13b는 뮤린 STRC 단백질의 C-말단 부분, 신호 펩티드 서열 및 C-인테인 (예를 들어, CFS-C-Strc-C-Int, 구축물 2, C-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 19)을 보여준다. 뉴클레오티드 서열은 신호 서열, C-인테인 서열 (인테인 단백질의 C-말단 단편을 코딩함), 3' Strc (야생형 Strc 코딩 서열의 3' 단편), 링커 서열 및 myc 태그 서열을 함유한다.
도 14는 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱에 사용되는 신호 펩티드 서열, C-인테인 및 STRC 단백질의 C-말단 부분을 코딩하는 도 13a 및 13b의 뉴클레오티드 서열을 함유하는 구축물의 개략적 표현을 보여준다.
도 15는 도 12a 및 12b에 제시된 뉴클레오티드 서열에 의해 코딩되는 신호 펩티드 서열, C-인테인, 인간 STRC 단백질의 C-말단 부분, 링커 서열 및 myc 태그를 함유하는 아미노산 서열 (서열식별번호: 18)을 보여준다.
도 16은 도 13a 및 13b에 제시된 뉴클레오티드 서열에 의해 코딩되는 신호 펩티드 서열, C-인테인, 뮤린 STRC 단백질의 C-말단 부분, 링커 서열 및 myc 태그를 함유하는 아미노산 서열 (서열식별번호: 20)을 보여준다.
도 17은 도 8a, 8b, 13a 및 13b의 서열에 의해 생성되고 도 9 및 14의 구축물에 의해 도시된 바와 같은 도 11 및 16의 시스테인 (C; Cys), 페닐알라닌 (F, Phe) 및 세린 (S; Ser)을 함유하는 명시된 CFS 분할 부위를 갖는 스테레오실린 (STRC) 단백질의 예측 구조를 보여준다.
도 18a 및 18b는 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 N-인테인 (예를 들어, CFS-N-Strc-N-Int, 구축물 1, N-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 51)을 보여준다. 뉴클레오티드 서열은 신호 서열, 5' Strc (야생형 Strc 코딩 서열의 5' 단편) 및 N-인테인 서열 (인테인 단백질의 N-말단 단편을 코딩함)을 함유한다.
도 19는 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱에 사용된 신호 펩티드 서열, STRC 단백질의 N-말단 부분 및 N-인테인을 코딩하는 도 18a 및 18b의 뉴클레오티드 서열을 함유하는 구축물의 개략적 표현을 보여준다.
도 20은 도 18a 및 18b에 제시된 뉴클레오티드 서열에 의해 코딩되는 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 N-인테인을 함유하는 아미노산 서열 (서열식별번호: 52)을 보여준다.
도 21a 및 21b는 STRC 단백질의 C-말단 부분, 신호 펩티드 서열 및 C-인테인 (예를 들어, CFS-C-Strc-C-Int, 구축물 1, C-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 53)을 보여준다. 뉴클레오티드 서열은 신호 서열, C-인테인 서열 (인테인 단백질의 C-말단 단편을 코딩함), 3' Strc (야생형 Strc 코딩 서열의 3' 단편), 링커 서열 및 myc 태그 서열을 함유한다.
도 22는 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱에 사용되는 신호 펩티드 서열, C-인테인 및 STRC 단백질의 C-말단 부분을 코딩하는 도 21a 및 21b의 뉴클레오티드 서열을 함유하는 구축물의 개략적 표현을 보여준다.
도 23은 도 21a 및 21b에 제시된 뉴클레오티드 서열에 의해 코딩되는 신호 펩티드 서열, C-인테인, STRC 단백질의 C-말단 부분, 링커 서열 및 myc 태그를 함유하는 아미노산 서열 (서열식별번호: 54)을 보여준다.
도 24는 도 8a, 8b, 13a 및 13b의 서열을 사용하여 레인 4에서 단리된 STRC 단백질의 웨스턴 블롯에 의해 입증된 바와 같이 및 도 9 및 14의 구축물 (AAV2/AAV9-Php.B-STRC-구축물 2)에 의해 도시된 바와 같이 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱 및 프로세싱을 확인시켜 준다.
도 25는 도 8a, 8b, 13a 및 13b의 서열을 사용하여 레인 6에서 단리된 STRC 단백질의 웨스턴 블롯에 의해 입증된 바와 같이 및 신호 서열이 결여된 레인 4와 대조적으로 신호 서열을 갖는 도 9 및 14의 구축물 (AAV2/AAV9-Php.B-STRC-구축물 2)에 의해 도시된 바와 같이 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱 및 프로세싱에서의 신호 서열의 유용성을 확인시켜 준다.
도 26은 야생형 (WT) 마우스 (StrcWT/WT) 및 STRC 녹아웃 마우스 (Strc-/-)와 비교하여 도 9 및 14의 구축물로 감염된 STRC 녹아웃 마우스 (Strc-/-)에서의 음압 수준 (데시벨, dB)의 회복에 의해 입증된 바와 같이 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱 및 프로세싱을 사용한 청력 상실의 회복을 보여준다.
도 27은 Strc 녹아웃 마우스에서 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱 시스템 (구축물 2: AAV2/AAV9-PHP.B-CMV-Strc-N; AAV2/AAV9-PHP.B-CMV-Strc-C)으로의 처리에 의한 청각 기능의 회복을 입증하는 ABR 및 DPOAE 결과를 보여준다.
도 28은 도 9에 도시된 STRC 단백질의 N-말단 부분을 코딩하는 구축물만을 사용한 경우 Strc 녹아웃 마우스에서의 청각 기능 회복의 결여를 입증하는 ABR 및 DPOAE 결과를 보여준다.
도 29는 도 14에 도시된 STRC 단백질의 C-말단 부분을 코딩하는 구축물만을 사용한 경우 Strc 녹아웃 마우스에서의 청각 기능 회복의 결여를 입증하는 ABR 및 DPOAE 결과를 보여준다.
도 30은 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱 시스템 (구축물 2: AAV2/AAV9-PHP.B-CMV-Strc-N; AAV2/AAV9-PHP.B-CMV-Strc-C)으로의 Strc 녹아웃 마우스의 처리 후 생체내에서의 시간 경과에 따른 ABR 및 DPOAE 결과를 보여준다.
도 31a-31c는 인테인-매개 단백질 재조합을 사용하는 이중 벡터 전략을 제공한다. 도 31a는 4개의 상이한 이중 벡터 변이체를 포함하는 생성된 8개의 AAV2 플라스미드를 제공한다. N-말단 및 C-말단 인테인을 4개의 변이체 각각에 대해 지시된 부위에서 인-프레임으로 융합시켰다. 변이체 1 및 2는 그의 분할 부위가 상이하며, 여기서 천연 시스테인은 위치 747 (변이체 1) 및 위치 970 (변이체 2)에 위치한다. 변이체 3 및 4는 각각 동일한 분할 부위 1 및 2를 가졌다. 추가로, 변이체 3 및 4는 C-인테인 서열의 상류에, C-말단 단편의 N-말단에 융합된 STRC의 N-말단에서 발견된 신호 서열을 가졌다. 인테인-매개 단백질 재조합은 전장 STRC 및 절제된 인테인 단편을 생성할 것으로 예측되었다. Myc 태그 (제시되지 않음)를 모든 C-말단 단편의 C-말단에 융합시켰다. 도 31b는 4개의 변이체에 대한 분할 부위 및 주위 아미노산 서열을 보여준다. 도 31c는 전장 STRC를 코딩하는 플라스미드 (레인 1), 비-형질감염된 대조군 (레인 2), 변이체 1 (레인 3) 및 변이체 3 (레인 5)의 C-말단 단편을 코딩하는 플라스미드 및 변이체 1 (레인 4) 및 변이체 3 (레인 6)에 대한 N- 및 C-단편 둘 다의 공동-형질감염으로 형질감염된 인간 배아 신장 (HEK) 293 세포로부터의 용해물의 대표적인 웨스턴 블롯 분석을 제공한다. 항-Myc 항체를 사용하여 C-말단 단편 (120 kD) 및 전장 STRC (220 kD)를 확인하였다.
도 32a-32g는 StrcΔ/Δ 마우스의 생성 및 특징화를 보여준다. 도 32a는 WT Strc의 파괴를 위한 CRISPR/Cas9 전략을 예시한다. 엑손 4를 표적화하도록 3개의 가이드 RNA (sgRNA)를 설계하였다. 유전자 파괴 전략은 249개의 뉴클레오티드의 결실 및 2개의 전위 및 역위 (947-1139 - 자주색 및 1758-1835 - 황색)를 생성하였으며, 이는 돌연변이 Strc 대립유전자에 조기 정지 코돈을 도입하였다. 도 32b는 게놈 DNA를 증폭시키는 데 사용된 PCR의 결과를 제공하며, 이는 겔 상에 전개되었을 때 WT (1kB) 및 돌연변이 Strc (751 bp) 대립유전자에 대해 명확한 밴드를 생성하였다. 도 32c-32d는 유모 다발을 조명하기 위해 알렉사488 2차 및 팔로이딘-알렉사555, 항-STRC 항체로 염색된 조직으로부터 취한 WT 및 StrcΔ/Δ 와우의 공초점 영상을 예시한다. 내유모 세포 (IHC) 및 3열의 외유모 세포 (OHC)가 가시적이다. 녹색 STRC 염색은 WT의 OHC 상에 존재하는 반면, 적색 액틴 염색은 WT 및 StrcΔ/Δ 둘 다의 IHC 상에 존재한다. 축척 막대 = 10 mm. 도 32e는 StrcΔ/+ (Het-흑색 원형) 및 StrcΔ/Δ (Homo-적색 마름모형) 마우스의 IHC 및 OHC로부터 측정된 평균 ± S.D. 감각 전달 전류 진폭을 보여준다. 도 32f는 StrcD/D 마우스 (n=6; 적색) 및 WT 마우스 (n=5; 흑색)로부터 수득된 평균 ± S.D. DPOAE 역치를 보여준다. 도 32g는 StrcΔ/Δ 마우스 (n=6; 적색) 및 WT 마우스 (n=5; 흑색)로부터 수득된 평균 ± S.D. ABR 역치를 예시한다.
도 33a-b는 이중 AAV 전달이 STRC 발현 및 유모 다발 형태를 회복시킨다는 것을 입증한다. 도 33a는 알렉사488 접합된 2차 (녹색) 및 알렉사546-팔로이딘 (적색)을 갖는 항-STRC 항체로 염색된 WT (좌측), StrcΔ/Δ (중간) 및 이중 벡터 주사된 StrcΔ/Δ (우측) 와우의 공초점 영상을 제공한다. 축척 막대 = 10 mm. 상부 열의 영상은 합병된 2개의 채널을 보여준다. 하부 열은 STRC 국재화 단독을 보여준다. 도 33b는 WT (상단), StrcΔ/Δ (중간) 및 이중 벡터 주사된 StrcΔ/Δ (하단) 외유모 세포 다발의 스캐닝 전자 현미경검사 영상을 보여준다. 조직을 수거하고, 고정시키고, 상기 나타낸 바와 같이 4 또는 12주에 영상화하였다. 축척 막대 = 5 mm (좌측 & 중간) 또는 2 mm (우측).
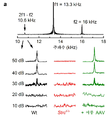
도 34a-34d는 이중 AAV 전달이 DPOAE 및 ABR 역치를 회복시킨다는 것을 보여준다. 도 34a는 WT 마우스 와우 (상부 트레이스)에서 자극 주파수 f1 (13.3 kHz) 및 f2 (16 kHz)에서의 2개의 주파수 성분 및 예측 주파수 2f1 - f2 (10.6 kHz)에서의 변조물을 나타낸 DPOAE 파형의 푸리에 분석을 제공한다. 하기 트레이스는 WT (좌측), StrcΔ/Δ (중간) 및 이중 벡터 주사된 StrcΔ/Δ (우측) 와우에 대한 확장된 주파수 및 진폭 스케일 상에서의 10 내지 50 dB의 음압 수준에 대한 변조물을 나타낸다. 볼드 트레이스는 DPOAE 역치를 나타낸다. 도 34b는 WT (흑색) 및 이중 벡터 주사된 StrcΔ/Δ 마우스 중 회복이 있는 마우스 (자주색) 및 회복이 없는 마우스 (StrcΔ/Δ; 적색; n=20; 상단 수평선)에 대한 (f2) 자극 주파수의 함수로서의 DPOAE 역치를 제공한다. 적색 및 자주색 선은 개체로부터의 데이터를 나타낸다. 평균 ± S.E.는 WT (흑색; n=5; 가장 하부의 선), 회복된 20마리의 이중 벡터 주사된 StrcΔ/Δ 마우스 (자주색; n=20; 상단으로부터 두번째 선) 및 5마리의 최상의 회복 마우스 (녹색; n=5; 상단으로부터 세번째 선)에 대해 제시된다. 도 34c는 25 내지 110 dB의 음압 수준에 의해 유발된, WT (좌측), StrcΔ/Δ (중간) 및 이중 벡터 주사된 StrcΔ/Δ (우측) 와우로부터 기록된 ABR 트레이스의 패밀리를 예시한다. 볼드 트레이스는 ABR 역치를 나타낸다. 도 34d는 WT (흑색; n=5; 가장 하부의 선) 및 이중 벡터 주사된 StrcΔ/Δ 마우스 중 회복이 있는 마우스 (자주색; n=20; 상단으로부터 두번째) 및 회복이 없는 마우스 (StrcΔ/Δ; 적색; n=20; 상단 선)에 대한 자극 주파수의 함수로서 플롯팅된 ABR 역치를 제공한다. 자주색 선은 개체로부터의 데이터를 나타낸다. 평균 ± S.E.는 WT (흑색; n=5; 가장 하부의 선), 이중 벡터 주사된 StrcΔ/Δ 마우스 중 회복이 있는 마우스 (자주색; n=20; 상단으로부터 두번째 선) 및 회복이 없는 마우스 (StrcΔ/Δ; 적색; n=20; 상단 선) 및 가장 양호한 회복을 갖는 마우스 (녹색; n=5; 상단으로부터 세번째 선)에 대해 제시된다.
도 2a-2c는 인간 STRC 단백질을 코딩하는 뉴클레오티드 서열, 신호 펩티드 서열, 링커 서열, Myc 태그를 코딩하는 서열 및 출발 및 정지 코돈 (서열식별번호: 33)을 보여준다.
도 3은 도 2a-2c에 제시된 뉴클레오티드 서열에 의해 코딩되는 신호 펩티드 서열, 인간 STRC 단백질 서열, 링커 서열 및 myc 태그를 함유하는 아미노산 서열 (서열식별번호: 36)을 보여준다.
도 4a-4d는 뮤린 STRC 단백질을 코딩하는 뉴클레오티드 서열, 신호 펩티드 서열, 링커 서열, Myc 태그를 코딩하는 서열 및 출발 및 정지 코돈 (서열식별번호: 38)을 보여준다.
도 5는 도 4a 내지 4d에 제시된 뉴클레오티드 서열에 의해 코딩되는 신호 펩티드 서열, 뮤린 STRC 단백질 서열, 링커 서열 및 Myc 태그를 함유하는 아미노산 서열 (서열식별번호: 39)을 보여준다.
도 6은 AAV2 역전된 말단 반복부, 프로모터 및 폴리-아데닐화 서열을 사용한 이중 AAV 인테인-매개 스테레오실린 단백질 트랜스-스플라이싱의 개략적 표현을 보여준다. 인테인 단편은 단백질 재조합을 매개하고, 그 자체를 절제하고, 나머지 STRC 단편 (엑스테인)을 펩티드 결합으로 연결한다.
도 7a 및 7b는 인간 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 스플라이스 공여자 서열 (예를 들어, N-인테인; CFS-N-Strc-N-Int, 구축물 2, N-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 5)을 보여준다. 뉴클레오티드 서열은 신호 서열, 5' Strc (야생형 Strc 코딩 서열의 5' 단편) 및 N-인테인 서열 (인테인 단백질의 N-말단 단편을 코딩함)을 함유한다.
도 8a 및 8b는 뮤린 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 N-인테인 (예를 들어, CFS-N-Strc-N-Int, 구축물 2, N-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 7)을 보여준다. 뉴클레오티드 서열은 신호 서열, 5' Strc (야생형 Strc 코딩 서열의 5' 단편) 및 N-인테인 서열 (인테인 단백질의 N-말단 단편을 코딩함)을 함유한다.
도 9는 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱에 사용되는 신호 펩티드 서열, STRC 단백질의 N-말단 부분 및 N-인테인을 코딩하는 도 8a 및 8b의 뉴클레오티드 서열을 함유하는 구축물의 개략적 표현을 보여준다.
도 10은 도 7a 및 7b에 제시된 뉴클레오티드 서열에 의해 코딩되는 인간 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 N-인테인을 함유하는 아미노산 서열 (서열식별번호: 6)을 보여준다.
도 11은 도 8a 및 8b에 제시된 뉴클레오티드 서열에 의해 코딩되는 뮤린 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 N-인테인을 함유하는 아미노산 서열 (서열식별번호: 8)을 보여준다.
도 12a 및 12b는 인간 STRC 단백질의 C-말단 부분, 신호 펩티드 서열 및 C-인테인 (예를 들어, CFS-C-Strc-C-Int, 구축물 2, C-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 17)을 보여준다. 뉴클레오티드 서열은 신호 서열, C-인테인 서열 (인테인 단백질의 C-말단 단편을 코딩함), 3' Strc (야생형 Strc 코딩 서열의 3' 단편), 링커 서열 및 myc 태그 서열을 함유한다.
도 13a 및 13b는 뮤린 STRC 단백질의 C-말단 부분, 신호 펩티드 서열 및 C-인테인 (예를 들어, CFS-C-Strc-C-Int, 구축물 2, C-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 19)을 보여준다. 뉴클레오티드 서열은 신호 서열, C-인테인 서열 (인테인 단백질의 C-말단 단편을 코딩함), 3' Strc (야생형 Strc 코딩 서열의 3' 단편), 링커 서열 및 myc 태그 서열을 함유한다.
도 14는 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱에 사용되는 신호 펩티드 서열, C-인테인 및 STRC 단백질의 C-말단 부분을 코딩하는 도 13a 및 13b의 뉴클레오티드 서열을 함유하는 구축물의 개략적 표현을 보여준다.
도 15는 도 12a 및 12b에 제시된 뉴클레오티드 서열에 의해 코딩되는 신호 펩티드 서열, C-인테인, 인간 STRC 단백질의 C-말단 부분, 링커 서열 및 myc 태그를 함유하는 아미노산 서열 (서열식별번호: 18)을 보여준다.
도 16은 도 13a 및 13b에 제시된 뉴클레오티드 서열에 의해 코딩되는 신호 펩티드 서열, C-인테인, 뮤린 STRC 단백질의 C-말단 부분, 링커 서열 및 myc 태그를 함유하는 아미노산 서열 (서열식별번호: 20)을 보여준다.
도 17은 도 8a, 8b, 13a 및 13b의 서열에 의해 생성되고 도 9 및 14의 구축물에 의해 도시된 바와 같은 도 11 및 16의 시스테인 (C; Cys), 페닐알라닌 (F, Phe) 및 세린 (S; Ser)을 함유하는 명시된 CFS 분할 부위를 갖는 스테레오실린 (STRC) 단백질의 예측 구조를 보여준다.
도 18a 및 18b는 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 N-인테인 (예를 들어, CFS-N-Strc-N-Int, 구축물 1, N-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 51)을 보여준다. 뉴클레오티드 서열은 신호 서열, 5' Strc (야생형 Strc 코딩 서열의 5' 단편) 및 N-인테인 서열 (인테인 단백질의 N-말단 단편을 코딩함)을 함유한다.
도 19는 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱에 사용된 신호 펩티드 서열, STRC 단백질의 N-말단 부분 및 N-인테인을 코딩하는 도 18a 및 18b의 뉴클레오티드 서열을 함유하는 구축물의 개략적 표현을 보여준다.
도 20은 도 18a 및 18b에 제시된 뉴클레오티드 서열에 의해 코딩되는 STRC 단백질의 N-말단 부분, 신호 펩티드 서열 및 N-인테인을 함유하는 아미노산 서열 (서열식별번호: 52)을 보여준다.
도 21a 및 21b는 STRC 단백질의 C-말단 부분, 신호 펩티드 서열 및 C-인테인 (예를 들어, CFS-C-Strc-C-Int, 구축물 1, C-부분)을 코딩하는 뉴클레오티드 서열 (서열식별번호: 53)을 보여준다. 뉴클레오티드 서열은 신호 서열, C-인테인 서열 (인테인 단백질의 C-말단 단편을 코딩함), 3' Strc (야생형 Strc 코딩 서열의 3' 단편), 링커 서열 및 myc 태그 서열을 함유한다.
도 22는 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱에 사용되는 신호 펩티드 서열, C-인테인 및 STRC 단백질의 C-말단 부분을 코딩하는 도 21a 및 21b의 뉴클레오티드 서열을 함유하는 구축물의 개략적 표현을 보여준다.
도 23은 도 21a 및 21b에 제시된 뉴클레오티드 서열에 의해 코딩되는 신호 펩티드 서열, C-인테인, STRC 단백질의 C-말단 부분, 링커 서열 및 myc 태그를 함유하는 아미노산 서열 (서열식별번호: 54)을 보여준다.
도 24는 도 8a, 8b, 13a 및 13b의 서열을 사용하여 레인 4에서 단리된 STRC 단백질의 웨스턴 블롯에 의해 입증된 바와 같이 및 도 9 및 14의 구축물 (AAV2/AAV9-Php.B-STRC-구축물 2)에 의해 도시된 바와 같이 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱 및 프로세싱을 확인시켜 준다.
도 25는 도 8a, 8b, 13a 및 13b의 서열을 사용하여 레인 6에서 단리된 STRC 단백질의 웨스턴 블롯에 의해 입증된 바와 같이 및 신호 서열이 결여된 레인 4와 대조적으로 신호 서열을 갖는 도 9 및 14의 구축물 (AAV2/AAV9-Php.B-STRC-구축물 2)에 의해 도시된 바와 같이 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱 및 프로세싱에서의 신호 서열의 유용성을 확인시켜 준다.
도 26은 야생형 (WT) 마우스 (StrcWT/WT) 및 STRC 녹아웃 마우스 (Strc-/-)와 비교하여 도 9 및 14의 구축물로 감염된 STRC 녹아웃 마우스 (Strc-/-)에서의 음압 수준 (데시벨, dB)의 회복에 의해 입증된 바와 같이 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱 및 프로세싱을 사용한 청력 상실의 회복을 보여준다.
도 27은 Strc 녹아웃 마우스에서 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱 시스템 (구축물 2: AAV2/AAV9-PHP.B-CMV-Strc-N; AAV2/AAV9-PHP.B-CMV-Strc-C)으로의 처리에 의한 청각 기능의 회복을 입증하는 ABR 및 DPOAE 결과를 보여준다.
도 28은 도 9에 도시된 STRC 단백질의 N-말단 부분을 코딩하는 구축물만을 사용한 경우 Strc 녹아웃 마우스에서의 청각 기능 회복의 결여를 입증하는 ABR 및 DPOAE 결과를 보여준다.
도 29는 도 14에 도시된 STRC 단백질의 C-말단 부분을 코딩하는 구축물만을 사용한 경우 Strc 녹아웃 마우스에서의 청각 기능 회복의 결여를 입증하는 ABR 및 DPOAE 결과를 보여준다.
도 30은 본원에 기재된 이중-AAV 인테인-매개 단백질 트랜스-스플라이싱 시스템 (구축물 2: AAV2/AAV9-PHP.B-CMV-Strc-N; AAV2/AAV9-PHP.B-CMV-Strc-C)으로의 Strc 녹아웃 마우스의 처리 후 생체내에서의 시간 경과에 따른 ABR 및 DPOAE 결과를 보여준다.
도 31a-31c는 인테인-매개 단백질 재조합을 사용하는 이중 벡터 전략을 제공한다. 도 31a는 4개의 상이한 이중 벡터 변이체를 포함하는 생성된 8개의 AAV2 플라스미드를 제공한다. N-말단 및 C-말단 인테인을 4개의 변이체 각각에 대해 지시된 부위에서 인-프레임으로 융합시켰다. 변이체 1 및 2는 그의 분할 부위가 상이하며, 여기서 천연 시스테인은 위치 747 (변이체 1) 및 위치 970 (변이체 2)에 위치한다. 변이체 3 및 4는 각각 동일한 분할 부위 1 및 2를 가졌다. 추가로, 변이체 3 및 4는 C-인테인 서열의 상류에, C-말단 단편의 N-말단에 융합된 STRC의 N-말단에서 발견된 신호 서열을 가졌다. 인테인-매개 단백질 재조합은 전장 STRC 및 절제된 인테인 단편을 생성할 것으로 예측되었다. Myc 태그 (제시되지 않음)를 모든 C-말단 단편의 C-말단에 융합시켰다. 도 31b는 4개의 변이체에 대한 분할 부위 및 주위 아미노산 서열을 보여준다. 도 31c는 전장 STRC를 코딩하는 플라스미드 (레인 1), 비-형질감염된 대조군 (레인 2), 변이체 1 (레인 3) 및 변이체 3 (레인 5)의 C-말단 단편을 코딩하는 플라스미드 및 변이체 1 (레인 4) 및 변이체 3 (레인 6)에 대한 N- 및 C-단편 둘 다의 공동-형질감염으로 형질감염된 인간 배아 신장 (HEK) 293 세포로부터의 용해물의 대표적인 웨스턴 블롯 분석을 제공한다. 항-Myc 항체를 사용하여 C-말단 단편 (120 kD) 및 전장 STRC (220 kD)를 확인하였다.
도 32a-32g는 StrcΔ/Δ 마우스의 생성 및 특징화를 보여준다. 도 32a는 WT Strc의 파괴를 위한 CRISPR/Cas9 전략을 예시한다. 엑손 4를 표적화하도록 3개의 가이드 RNA (sgRNA)를 설계하였다. 유전자 파괴 전략은 249개의 뉴클레오티드의 결실 및 2개의 전위 및 역위 (947-1139 - 자주색 및 1758-1835 - 황색)를 생성하였으며, 이는 돌연변이 Strc 대립유전자에 조기 정지 코돈을 도입하였다. 도 32b는 게놈 DNA를 증폭시키는 데 사용된 PCR의 결과를 제공하며, 이는 겔 상에 전개되었을 때 WT (1kB) 및 돌연변이 Strc (751 bp) 대립유전자에 대해 명확한 밴드를 생성하였다. 도 32c-32d는 유모 다발을 조명하기 위해 알렉사488 2차 및 팔로이딘-알렉사555, 항-STRC 항체로 염색된 조직으로부터 취한 WT 및 StrcΔ/Δ 와우의 공초점 영상을 예시한다. 내유모 세포 (IHC) 및 3열의 외유모 세포 (OHC)가 가시적이다. 녹색 STRC 염색은 WT의 OHC 상에 존재하는 반면, 적색 액틴 염색은 WT 및 StrcΔ/Δ 둘 다의 IHC 상에 존재한다. 축척 막대 = 10 mm. 도 32e는 StrcΔ/+ (Het-흑색 원형) 및 StrcΔ/Δ (Homo-적색 마름모형) 마우스의 IHC 및 OHC로부터 측정된 평균 ± S.D. 감각 전달 전류 진폭을 보여준다. 도 32f는 StrcD/D 마우스 (n=6; 적색) 및 WT 마우스 (n=5; 흑색)로부터 수득된 평균 ± S.D. DPOAE 역치를 보여준다. 도 32g는 StrcΔ/Δ 마우스 (n=6; 적색) 및 WT 마우스 (n=5; 흑색)로부터 수득된 평균 ± S.D. ABR 역치를 예시한다.
도 33a-b는 이중 AAV 전달이 STRC 발현 및 유모 다발 형태를 회복시킨다는 것을 입증한다. 도 33a는 알렉사488 접합된 2차 (녹색) 및 알렉사546-팔로이딘 (적색)을 갖는 항-STRC 항체로 염색된 WT (좌측), StrcΔ/Δ (중간) 및 이중 벡터 주사된 StrcΔ/Δ (우측) 와우의 공초점 영상을 제공한다. 축척 막대 = 10 mm. 상부 열의 영상은 합병된 2개의 채널을 보여준다. 하부 열은 STRC 국재화 단독을 보여준다. 도 33b는 WT (상단), StrcΔ/Δ (중간) 및 이중 벡터 주사된 StrcΔ/Δ (하단) 외유모 세포 다발의 스캐닝 전자 현미경검사 영상을 보여준다. 조직을 수거하고, 고정시키고, 상기 나타낸 바와 같이 4 또는 12주에 영상화하였다. 축척 막대 = 5 mm (좌측 & 중간) 또는 2 mm (우측).
도 34a-34d는 이중 AAV 전달이 DPOAE 및 ABR 역치를 회복시킨다는 것을 보여준다. 도 34a는 WT 마우스 와우 (상부 트레이스)에서 자극 주파수 f1 (13.3 kHz) 및 f2 (16 kHz)에서의 2개의 주파수 성분 및 예측 주파수 2f1 - f2 (10.6 kHz)에서의 변조물을 나타낸 DPOAE 파형의 푸리에 분석을 제공한다. 하기 트레이스는 WT (좌측), StrcΔ/Δ (중간) 및 이중 벡터 주사된 StrcΔ/Δ (우측) 와우에 대한 확장된 주파수 및 진폭 스케일 상에서의 10 내지 50 dB의 음압 수준에 대한 변조물을 나타낸다. 볼드 트레이스는 DPOAE 역치를 나타낸다. 도 34b는 WT (흑색) 및 이중 벡터 주사된 StrcΔ/Δ 마우스 중 회복이 있는 마우스 (자주색) 및 회복이 없는 마우스 (StrcΔ/Δ; 적색; n=20; 상단 수평선)에 대한 (f2) 자극 주파수의 함수로서의 DPOAE 역치를 제공한다. 적색 및 자주색 선은 개체로부터의 데이터를 나타낸다. 평균 ± S.E.는 WT (흑색; n=5; 가장 하부의 선), 회복된 20마리의 이중 벡터 주사된 StrcΔ/Δ 마우스 (자주색; n=20; 상단으로부터 두번째 선) 및 5마리의 최상의 회복 마우스 (녹색; n=5; 상단으로부터 세번째 선)에 대해 제시된다. 도 34c는 25 내지 110 dB의 음압 수준에 의해 유발된, WT (좌측), StrcΔ/Δ (중간) 및 이중 벡터 주사된 StrcΔ/Δ (우측) 와우로부터 기록된 ABR 트레이스의 패밀리를 예시한다. 볼드 트레이스는 ABR 역치를 나타낸다. 도 34d는 WT (흑색; n=5; 가장 하부의 선) 및 이중 벡터 주사된 StrcΔ/Δ 마우스 중 회복이 있는 마우스 (자주색; n=20; 상단으로부터 두번째) 및 회복이 없는 마우스 (StrcΔ/Δ; 적색; n=20; 상단 선)에 대한 자극 주파수의 함수로서 플롯팅된 ABR 역치를 제공한다. 자주색 선은 개체로부터의 데이터를 나타낸다. 평균 ± S.E.는 WT (흑색; n=5; 가장 하부의 선), 이중 벡터 주사된 StrcΔ/Δ 마우스 중 회복이 있는 마우스 (자주색; n=20; 상단으로부터 두번째 선) 및 회복이 없는 마우스 (StrcΔ/Δ; 적색; n=20; 상단 선) 및 가장 양호한 회복을 갖는 마우스 (녹색; n=5; 상단으로부터 세번째 선)에 대해 제시된다.
본 개시내용의 상세한 실시양태가 본원에 개시되지만; 개시된 실시양태는 단지 다양한 형태로 구현될 수 있는 개시내용의 예시인 것으로 이해되어야 한다. 추가로, 본 개시내용의 다양한 실시양태와 관련하여 주어진 각각의 실시예는 예시적인 것으로 의도되고, 제한적인 것으로 의도되지 않는다.
스테레오실린 (STRC)의 발현을 통해 청력을 회복시키는 조성물 및 방법이 본원에 제공된다. 하나는 신호 서열, 유전자 코딩 서열의 5' 말단 단편 및 인테인의 아미노 말단 단편 (N-인테인, 또한 스플릿 인테인-N으로도 공지됨)을 코딩하는 서열을 포함하고, 하나는 신호 서열, 인테인의 카르복시 말단 단편 (C-인테인, 또한 스플릿 인테인-C로도 공지됨)을 코딩하는 서열 및 유전자 코딩 서열의 3' 말단 단편을 포함하는 2개의 별개의 AAV 입자 또는 벡터를 사용한 관심 유전자로의 처리가 제공된다.
달리 정의되지 않는 한, 본원에 사용된 모든 기술 과학 용어는 본 발명이 속하는 기술분야의 통상의 기술자에 의해 통상적으로 이해되는 의미를 갖는다. 하기 참고문헌은 관련 기술분야의 통상의 기술자에게 본 발명에 사용된 많은 용어의 일반적 정의를 제공한다: 문헌 [Singleton et al., Dictionary of Microbiology and Molecular Biology (2nd ed. 1994); The Cambridge Dictionary of Science and Technology (Walker ed., 1988); The Glossary of Genetics, 5th Ed., R. Rieger et al. (eds.), Springer Verlag (1991); 및 Hale & Marham, The Harper Collins Dictionary of Biology (1991)].
정의
본원에 사용된 모든 용어는 달리 제공되지 않는 한 관련 기술분야에서의 그의 통상의 의미를 갖는 것으로 의도된다. 모든 농도는, 달리 정의되지 않는 한, 국소 조성물의 전체 중량에 대한 명시된 성분의 중량 백분율에 대한 것이다.
본원에 사용된 단수형은 하나 이상을 의미할 것이다. 단어 "포함하는"과 함께 사용되는 경우에 본원에 사용된 단수형 단어는 하나 또는 하나 초과를 의미한다. 본원에 사용된 "또 다른"은 적어도 두번째 이상을 의미한다.
"아데노-연관 바이러스" (AAV)는 인간 및 일부 다른 영장류 종을 감염시킬 수 있는 소형 바이러스이다. AAV를 사용하는 벡터는 숙주 세포의 게놈 내로 통합되지 않으면서 분열 및 휴지 세포를 감염시킬 수 있다. 이들 특색은 AAV를 유전자 요법 바이러스 벡터에 대한 매력적인 후보로 만든다.
"AAV9-php.b 벡터"는 세포, 예를 들어 내이의 세포를 형질감염시킬 수 있는 AAV9-php.b 폴리뉴클레오티드 또는 그의 단편을 포함하는 바이러스 벡터인 아데노-연관 바이러스 혈청형 9를 의미한다. 한 실시양태에서, AAV9-php.b 벡터는 세포의 적어도 70% 이상 (예를 들어, 75%, 80%, 85%, 90%, 95%, 97%, 99%, 100%)을 형질감염시킨다. 또 다른 실시양태는 AAV9-php.b 벡터를 대상체의 내이에 투여하거나 AAV9-php.b 벡터를 시험관내에서 내이로부터 유래된 세포와 접촉시킨 후에 내유모 세포 및/또는 외유모 세포의 적어도 70% 이상 (예를 들어, 75%, 80%, 85%, 90%, 95%, 97%, 99%, 100%)을 형질감염시킬 수 있는 AAV9-php.b 폴리뉴클레오티드 또는 그의 단편을 포함하는 AAV9-php.b 벡터에 관한 것일 수 있다. 다른 실시양태에서, 내유모 세포의 적어도 85% (예를 들어, 90%, 95%, 100%) 및/또는 외유모 세포의 적어도 85% (예를 들어, 90%, 95%, 100%)가 AAV9-php.b 벡터로 형질감염된다. 형질감염 효율은 마우스 모델에서 표지 또는 태그 (예를 들어, 녹색 형광 단백질 (GFP)을 코딩하는 유전자)를 사용하여 평가될 수 있다.
본 개시내용의 한 실시양태는 목적하는 단백질을 코딩하는 뉴클레오티드 서열을 포함하는 적어도 1개의 벡터 (예를 들어, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터 (예를 들어, 렌티바이러스), 아데노바이러스, AAV, AAV 게놈)에 관한 것일 수 있다 (도 1). 도 2a-2c는 하기와 같은 5'에서 3' 방향으로 인간 STRC 유전자 코딩 서열 (서열식별번호: 1) (도 3에서 인간 STRC 단백질 서열 (대문자)인 서열식별번호: 2를 코딩함)을 함유하는 뉴클레오티드 서열 (서열식별번호: 33)을 보여준다:
추가 실시양태는 하기와 같은 5'에서 3' 방향으로 뮤린 STRC 유전자 코딩 서열 (서열식별번호: 3) (도 5에서 뮤린 STRC 단백질 서열인 서열식별번호: 4를 코딩함)을 포함하는 적어도 1개의 벡터 (예를 들어, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈) (예를 들어, 도 4a-4d; 서열식별번호: 38 참조)에 관한 것일 수 있다:
본 개시내용의 또 다른 실시양태는, 5'에서 3' 방향으로: 부분 코딩 서열의 5'-말단에 있는 신호 서열 (예를 들어, 서열식별번호: 10을 코딩하는 서열식별번호: 9; 또는 서열식별번호: 12를 코딩하는 서열식별번호: 11); 관심 단백질 (예를 들어, STRC; 서열식별번호: 15; 서열식별번호: 16)의 아미노 말단 (N-말단) 부분을 코딩하는 부분 코딩 서열; 부분 코딩 서열에 플랭킹되거나 인접할 수 있는 스플라이스 공여자 서열을 코딩하는 하류 서열 (예를 들어, N-말단 인테인 (N-인테인); 서열식별번호: 14를 코딩하는 서열식별번호: 13)을 포함하는 제1 뉴클레오티드 서열 (예를 들어, 서열식별번호: 6을 코딩하는 서열식별번호: 5; 서열식별번호: 8을 코딩하는 서열식별번호: 7)을 포함하는 제1 벡터 (예를 들어, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈); 및 5'에서 3' 방향으로: 신호 서열 (예를 들어, 인간 서열식별번호: 10을 코딩하는 서열식별번호: 9; 또는 뮤린 서열식별번호: 12를 코딩하는 서열식별번호: 11), 신호 서열이 그의 상류일 수 있는 스플라이스 수용자 서열 (예를 들어, C-말단 인테인 (C-인테인); 서열식별번호: 22를 코딩하는 서열식별번호: 21), 그에 바로 인접하여 위치하거나 플랭킹된 관심 단백질의 전장 코딩 서열의 나머지 부분, 즉 관심 단백질의 C-말단 부분 (예를 들어, STRC; 인간 서열식별번호: 23; 서열식별번호: 24)을 코딩하는 하류 부분 코딩 서열을 포함하는 제2 뉴클레오티드 서열 (예를 들어, 서열식별번호: 18을 코딩하는 서열식별번호: 17; 서열식별번호: 20을 코딩하는 서열식별번호: 19)을 포함하는 제2 벡터 (예를 들어, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈)를 제공할 수 있다. 세포 (예를 들어, 숙주 세포, 포유동물 (예를 들어, 인간, 개, 고양이, 말, 뮤린))에서 발현되는 경우에, 제1 벡터 및 제2 벡터는 각각 관심 단백질의 그의 각각의 부분 (예를 들어, N-STRC, C-STRC)을 발현할 수 있으며, 이는 전장 관심 단백질 (예를 들어, STRC; 서열식별번호: 25; 서열식별번호: 26)을 형성한다.
또 다른 실시양태는 관심 단백질 (예를 들어, STRC)의 아미노 말단 (N-말단) 부분을 코딩하는 부분 코딩 서열, 부분 코딩 서열의 5'-말단에 있는 신호 서열, 부분 코딩 서열에 플랭킹되거나 인접할 수 있는 스플라이스 공여자 서열 (예를 들어, N-말단 인테인 (N-인테인))을 코딩하는 하류 서열, 스플라이스 공여자 서열에 플랭킹되거나 인접한 하류 3'ITR 서열을 함유하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터 (예를 들어, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈)를 제공할 수 있다 (예를 들어, AAV9-php.B-Prot-trans/공여자). 관심 단백질 (예를 들어, STRC)의 나머지 C-말단 부분을 코딩하는 하류 부분 코딩 서열에 바로 인접하여 위치하거나 플랭킹된 스플라이스 수용자 서열 (예를 들어, C-말단 인테인 (C-인테인))의 상류일 수 있는 신호 서열의 상류의 5'ITR 서열을 함유하는 제2 뉴클레오티드 서열이며, 추가로 관심 단백질의 C-말단 부분을 코딩하는 부분 코딩 서열의 하류에 C-말단 myc 태그를 함유할 수 있는 제2 뉴클레오티드 서열을 포함하는 제2 벡터 (예를 들어, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈)를 제공할 수 있다 (예를 들어, AAV9-phpB-Prot-trans/수용자). 전장 관심 mRNA (예를 들어, STRC mRNA)는 2개의 벡터 (예를 들어, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈)로 공동-감염된 세포에서 2개의 트랜스스플라이싱 플라스미드 사이의 머리-대-꼬리 재조합 (5'에서 3' 말단 대 5'에서 3' 말단), 전사 및 역전된 말단 반복부 (ITR) 접합부에 걸친 후속 스플라이싱에 의해 형성될 수 있다.
관심 단백질이, 예를 들어 스테레오실린 (STRC) 단백질인 "관심 단백질의 N-말단 부분 또는 단편을 코딩하는 서열"은 STRC의 N-말단 부분 또는 단편의 부분 코딩 서열을 의미하며, 여기서 일부 경우에, "STRC의 N-말단 부분 또는 단편을 코딩하는 서열"은 STRC의 N-말단 부분 또는 단편의 부분 코딩 서열 (대문자)의 상류의 신호 펩티드 코딩 서열을 코딩하는 서열 (소문자, 이탤릭체 및 밑줄표시)을 포함할 수 있다. 일부 실시양태에서, "스테레오실린 (STRC)의 N-말단 단편을 코딩하는 서열"은 신호 펩티드 코딩 서열을 코딩하는 뉴클레오티드 서열을 포함하지 않을 수 있다. 또 다른 실시양태는 그의 C-말단 단부에서 인테인의 N-말단 부분 또는 단편 (N-인테인) (볼드체 및 밑줄표시)에 융합된 "STRC의 N-말단 단편 또는 부분을 코딩하는 서열"을 포함하는 뉴클레오티드 서열을 제공할 수 있으며, 여기서 5' 말단의 뉴클레오티드 서열은 "ATG" 개시 코돈 (볼드체)으로 시작하고 정지 코돈 (대문자, 이탤릭체 및 밑줄표시)으로 끝난다.
"STRC의 N-말단 부분 또는 단편을 코딩하는 서열"을 포함하는 예시적인 인간 뉴클레오티드 서열은 하기와 같을 수 있다:
"STRC의 N-말단 부분 또는 단편을 코딩하는 서열"을 포함하는 또 다른 예시적인 뮤린 뉴클레오티드 서열은 하기와 같을 수 있다:
관심 단백질이, 예를 들어 STRC 단백질인 "관심 단백질의 N-말단 부분 또는 단편"은 스테레오실린 (STRC) 폴리펩티드의 N-말단 부분 또는 단편의 아미노산 서열을 의미한다. 예를 들어, STRC의 N-말단 단편의 아미노산 서열은 ATG 개시 코돈에 의해 코딩되는 메티오닌 (M) (N-말단 단부에서 볼드체)으로 시작하는 N-말단 단부에 신호 펩티드 서열 (예를 들어, 22개 아미노산) (소문자, 이탤릭체 및 밑줄표시)을 포함할 수 있다. "STRC 단백질의 N-말단 부분 또는 단편"을 포함하는 아미노산 서열은 인테인의 N-말단 단편 (N-인테인) (볼드체 및 밑줄표시)의 하류 및/또는 그에 인접한 것을 추가로 포함할 수 있다. 또 다른 실시양태에서, "STRC 단백질의 N-말단 부분 또는 단편"은 신호 펩티드 서열이 없는 STRC의 N-말단 단편의 아미노산 서열을 의미한다.
인간 "STRC 단백질의 N-말단 부분 또는 단편"을 포함하는 예시적인 아미노산 서열은 하기와 같을 수 있다:
뮤린 "STRC 단백질의 N-말단 부분 또는 단편"을 포함하는 또 다른 예시적인 아미노산 서열은 하기와 같을 수 있다:
예시적인 "N-말단 STRC 폴리펩티드" 서열이 각각 인간 및 뮤린에 대해 하기에 제공된다 (N-말단에서 C-말단 방향으로).
ATG 개시 코돈 또는 신호 펩티드 서열에 의해 코딩되는 메티오닌을 포함하지 않는 예시적인 인간 N-말단 STRC 폴리펩티드 서열 (N-말단에서 C-말단 방향)이 하기에 제공된다 (N-말단에서 C-말단 방향):
ATG 개시 코돈 또는 신호 펩티드 서열에 의해 코딩되는 메티오닌을 포함하지 않는 또 다른 예시적인 뮤린 N-말단 STRC 폴리펩티드 서열 (N-말단에서 C-말단 방향)이 하기에 제공된다 (17개-잔기 소수성 영역은 밑줄표시됨) (N-말단에서 C-말단 방향):
"스테레오실린 (STRC)의 C-말단 부분 또는 단편을 코딩하는 서열"은 STRC의 C-말단 부분 또는 단편의 부분 코딩 서열을 의미한다. 한 실시양태는 5' 말단에서 "ATG" 개시 코돈 (5' 말단에서 볼드체), "STRC 단백질의 C-말단 부분 또는 단편을 코딩하는 뉴클레오티드 서열의 상류에 플랭킹된 인테인의 C-말단 단편 (C-인테인)을 코딩하는 서열 (볼드체 및 밑줄표시)의 상류에 플랭킹된 신호 펩티드 코딩 서열을 코딩하는 서열 (소문자, 이탤릭체 및 밑줄표시)을 포함하는 뉴클레오티드 서열을 제공할 수 있다. 또 다른 실시양태는 하류 링커 서열 (볼드체 및 이탤릭체), Myc 태그 (소문자) 및 정지 코돈 (대문자, 이탤릭체 및 밑줄표시)을 갖는 STRC의 C-말단 부분 또는 단편을 코딩하는 뉴클레오티드 서열을 추가로 제공할 수 있다.
"STRC의 C-말단 부분 또는 단편을 코딩하는 서열"을 포함하는 예시적인 인간 뉴클레오티드 서열은 하기와 같을 수 있다:
"STRC의 C-말단 부분 또는 단편을 코딩하는 서열"을 포함하는 예시적인 뮤린 뉴클레오티드 서열은 하기와 같을 수 있다:
"STRC 단백질의 C-말단 부분 또는 단편"은 스테레오실린 (STRC) 폴리펩티드의 C-말단 부분 또는 단편의 아미노산 서열을 의미한다. "STRC 단백질의 C-말단 부분 또는 단편"을 포함하는 아미노산 서열은 그 앞에, N-말단에서 C-말단 방향으로, ATG 개시 코돈에 의해 코딩되는 메티오닌 (M) (N-말단 단부에서 볼드체), 신호 펩티드 서열 (소문자, 이탤릭체 및 밑줄표시) 및 인테인의 C-말단 단편 (C-인테인) (볼드체 및 밑줄표시)이 선행할 수 있다. 아미노산 서열은 "STRC 단백질의 C-말단 부분 또는 단편"의 하류에 링커 서열 (볼드체 및 이탤릭체) 및 Myc 태그 (소문자)를 추가로 포함할 수 있다.
인간 "STRC 단백질의 C-말단 부분 또는 단편"을 포함하는 예시적인 아미노산 서열은 하기와 같을 수 있다:
뮤린 "STRC 단백질의 C-말단 부분 또는 단편"을 포함하는 또 다른 예시적인 아미노산 서열은 하기와 같을 수 있다:
예시적인 "C-말단 STRC 폴리펩티드" 서열이 각각 인간 및 뮤린에 대해 하기에 (N-말단에서 C-말단 방향으로) 제공된다.
신호 펩티드 서열을 포함하지 않는 STRC 단백질의 예시적인 인간 C-말단 부분은 하기와 같을 수 있다:
신호 펩티드 서열을 포함하지 않지만 밑줄표시된 바와 같은 적어도 16개 잔기의 소수성 영역을 포함하는 STRC 단백질의 예시적인 뮤린 C-말단 부분은 하기와 같을 수 있다:
STRC 단백질의 N-말단 부분 및 STRC 단백질의 C-말단 부분의 라이게이션은, 예컨대 펩티드 결합을 통해 발생하여, 전장 STRC 단백질을 생성할 수 있다.
"인테인"은 단백질 스플라이싱으로 공지된 과정에서 그 자체를 절제하고 나머지 단편 (엑스테인)을 펩티드 결합으로 연결시킬 수 있는 단백질의 단편이다. 인테인은 또한 "단백질 인트론"으로 지칭된다. 인테인이 그 자체를 절제하고 단백질의 나머지 부분을 연결하는 과정은 본원에서 "단백질 스플라이싱" 또는 "인테인-매개 단백질 스플라이싱"으로 지칭된다. 일부 실시양태에서, 전구체 단백질의 인테인 (인테인-매개 단백질 스플라이싱 전의 인테인 함유 단백질)은 2개의 유전자로부터 유래한다. 이러한 인테인은 본원에서 스플릿 인테인 (예를 들어, 스플릿 인테인-N 및 스플릿 인테인-C)으로 지칭된다. 예를 들어, 시아노박테리아에서, DNA 폴리머라제 III의 촉매 서브유닛인 DnaE는 2개의 별개의 유전자 dnaE-n 및 dnaE-c에 의해 코딩된다. dnaE-n 유전자에 의해 코딩되는 인테인은 본원에서 "인테인-N"으로 지칭될 수 있다. dnaE-c 유전자에 의해 코딩되는 인테인은 본원에서 "인테인-C"로 지칭될 수 있다.
다른 인테인 시스템이 또한 사용될 수 있다. 예를 들어, dnaE 인테인, Cfa-N (예를 들어, 스플릿 인테인-N) 및 Cfa-C (예를 들어, 스플릿 인테인-C) 인테인 쌍에 기초한 합성 인테인이 기재되었다 (예를 들어, 본원에 참조로 포함된 문헌 [Stevens et al., J Am Chem Soc. 2016 Feb. 24; 138(7):2162-5]). 본 개시내용에 따라 사용될 수 있는 인테인 쌍의 비제한적 예는 Cfa DnaE 인테인, Ssp GyrB 인테인, Ssp DnaX 인테인, Ter DnaE3 인테인, Ter ThyX 인테인, Rma DnaB 인테인 및 Cne Prp8 인테인 (예를 들어, 본원에 참조로 포함된 미국 특허 번호 8,394,604에 기재된 바와 같음)을 포함한다.
"myc 태그"는 c-myc 유전자로부터 유래된 폴리펩티드 단백질을 의미하며, 여기서 합성 펩티드 서열 (즉, EQKLISEEDL (서열식별번호: 27))은 인간 c-myc 단백질의 C-말단 아미노산 (410-419)에 상응한다. 이러한 태그는 단백질 단리 (예를 들어, 웨스턴 블롯팅, 면역형광, 면역침전)와 같은, 그러나 이에 제한되지는 않는 추가의 연구를 가능하게 한다.
예시적인 AAV9-php.b 벡터의 서열이 하기에 제공된다. 일부 실시양태에서, AAV9-php.b 벡터 (5'에서 3')는 하기에 대해 적어도 70% 이상 (예를 들어, 75%, 80%, 85%, 90%, 95%, 97%, 100%) 동일성의 뉴클레오티드 서열을 제공할 수 있다:
"투여하다"는 대상체에게 본원에 기재된 1개 이상의 조성물, 구축물 또는 바이러스 벡터를 제공하는 것을 의미한다. 예로서 및 비제한적으로, 투여는, 예를 들어 와우 내로의 주사에 의해 수행될 수 있다. 돌연변이에 의해 영향을 받는 세포에 조성물을 전달하는 다른 경로가 사용될 수 있다 (예를 들어, 정맥내, 직접 주사, 피하, 혈관 및/또는 비-혈관 정맥내). 투여는, 예를 들어 볼루스 주사에 의해 또는 시간 경과에 따른 점진적 관류에 의해 이루어질 수 있다.
"작용제"는 임의의 소분자 화학적 화합물, 항체, 핵산 분자 또는 폴리펩티드 또는 그의 단편을 의미한다.
"변경"은 표준 공지된 방법, 예컨대 본원에 기재된 방법에 의해 검출된 바와 같은 유전자 또는 폴리펩티드의 발현 수준 또는 활성의 변화 (증가 또는 감소)를 의미한다. 본원에 사용된 변경은 10% 이상 (예를 들어, 20%, 25%, 30%, 40%, 50%)의 발현 수준의 변화를 포함할 수 있다.
"호전시키다"는 질환 또는 상태의 발생 또는 진행을 감소, 저하, 억제, 약화, 경감, 정지 또는 안정화시키는 것을 의미한다. 예시적인 질환 또는 상태는 임의의 질환, 예컨대 유전자 돌연변이와 연관된 것을 포함할 수 있다. 한 실시양태에서, 질환은 우성 돌연변이 또는 열성 돌연변이, 예를 들어 비제한적으로, 난청, 상염색체 열성 1A (DFNB1A); 난청, 상염색체 열성 1B (DFNB1B); 난청, 상염색체 열성 2 (DFNB2); 난청, 상염색체 열성 4 (DFNB4); 난청, 상염색체 열성 6 (DFNB6); 난청, 상염색체 열성 7 (DFNB7); 난청, 상염색체 열성 8 (DFNB8); 난청, 상염색체 열성 9 (DFNB9); 난청, 상염색체 열성 10 (DFNB10); 난청, 상염색체 열성 16 (DFNB16); 난청, 상염색체 열성 24 (DFNB24); 난청, 상염색체 열성 25 (DFNB25); 난청, 상염색체 열성 59 (DFNB59); 난청, 상염색체 열성 98 (DFNB98); 난청, 상염색체 열성 110 (DFNB110); 선천성 이상각화증, 상염색체 열성 5 (DKCB5); 난청, 상염색체 우성 2B (DFNA2B); 난청, 상염색체 우성 3A (DFNA3A); 난청, 상염색체 우성 9 (DFNA9); 난청, 상염색체 우성 30 (DFNA30); 난청, 상염색체 우성 36 (DFNA36); 상염색체 우성 고립성 신경감각 난청 유형 (DFNA); 선천성 이상각화증, 상염색체 우성 4; 난청, 상염색체 우성 비증후군성 감각신경 (NSSHL); 볼프람-유사 증후군, 상염색체 우성 (WFSL)과 연관될 수 있다.
본원에 기재된 이중-벡터 시스템이 치료할 수 있는 추가의 질환 또는 상태는 불완전 상아질발생증 (DGI) 1; 난청, 상염색체 열성 16, 난청-불임 증후군 (DIS), CATSPER-관련 남성 불임증; 정자발생 실패 7 (SPGF7); 어셔 증후군, 유형 I (USH1); 블룸 증후군 (BLM); 총배설강 외번증; 펜드레드 증후군 (PDS); 뇌회형 맥락막 망막 위축 (GACR); 백내장 41 (CTRCT41); 전립선암; 및 유방암을 포함할 수 있으나 이에 제한되지는 않는다.
본 개시내용은 관심 물질을 보유하거나 보유할 수 있는 임의의 세포인 세포 (예를 들어, 숙주 세포)를 제공할 수 있다. 종종 숙주 세포는 포유동물 세포 (예를 들어, 인간, 개, 고양이, 말, 뮤린)이다. 숙주 세포는, 예를 들어 AAV 구축물, AAV 플라스미드, 헬퍼 구축물, 보조 기능 벡터 등을 수용할 수 있다. 본원에 사용될 수 있는 숙주 세포는 형질감염된 원래 세포의 자손을 포함한다. 본 개시내용의 "숙주 세포"는 또한 외인성 DNA 서열로 형질감염된 세포를 지칭할 수 있다. 단일 모 세포의 자손은 자연적, 비의도적 또는 고의적 돌연변이의 관점에서, 원래 모 세포와 형태학 또는 게놈 또는 총 DNA 상보체가 완전히 동일하지 않을 수 있다. 본원에 사용된 용어 "형질감염"은 세포에 의한 외래 DNA의 흡수를 지칭할 수 있고, 세포는 외인성 DNA가 세포 막 내부에 도입된 경우에 "형질감염된" 것이다. 다수의 형질감염 기술이 일반적으로 관련 기술분야에 공지되어 있다. 예를 들어, 문헌 [Graham et al. (1973) Virology, 52:456, Sambrook et al. (1989) Molecular Cloning, a laboratory manual, Cold Spring Harbor Laboratories, New York, Davis et al. (1986) Basic Methods in Molecular Biology, Elsevier, and Chu et al. (1981) Gene 13:197]을 참조한다. 이러한 기술을 사용하여 1개 이상의 외인성 핵산, 예컨대 뉴클레오티드 통합 벡터 및 다른 핵산 분자를 적합한 숙주 세포 내로 도입할 수 있다.
"핵산", "뉴클레오티드 서열" 및 "폴리뉴클레오티드 서열"은 단일- 또는 이중-가닥 형태의 데옥시리보뉴클레오티드 또는 리보뉴클레오티드 중합체를 의미하며, 달리 제한되지 않는 한, 자연 발생 뉴클레오티드와 유사한 방식으로 기능할 수 있는 자연 뉴클레오티드의 공지된 유사체를 포괄한다.
용어 "실질적으로 상동인", "실질적으로 동일한" 또는 "실질적으로 상응하는"은 선택된 핵산 또는 아미노산 서열이 선택된 참조 핵산 또는 아미노산 서열과 비교하여 적어도 70% 서열 동일성을 갖는 것인 핵산 또는 아미노산 서열의 특징을 지칭한다. 선택된 서열 및 참조 서열은 적어도 75% 이상 (예를 들어, 76%, 77%, 78%, 79%, 80%, 81%, 82%, 83%, 84%, 85%, 86%, 87%, 88%, 89%, 90%, 91%, 92%, 93%, 94%, 95%, 96%, 97%, 98%, 99%, 100%)의 서열 동일성을 가질 수 있다.
서열 동일성 또는 상동성은 비교되는 서열의 전체 길이에 걸쳐 결정될 수 있거나 또는 선택된 참조 서열의 길이보다 총 25% 이하 (예를 들어, 20%, 15%, 10%,5%)일 수 있는 서열의 단편에 의해 결정될 수 있다. 참조 서열은 보다 큰 서열의 부분, 예를 들어 유전자 또는 플랭킹 서열의 부분, 또는 염색체의 반복 부분일 수 있다. 2개 이상의 폴리뉴클레오티드 서열은 전형적으로 적어도 18-25개의 뉴클레오티드, 적어도 26-35개의 뉴클레오티드 또는 적어도 40개 (예를 들어, 50, 60, 70, 80, 90, 100, 500, 1000, 1500, 2000)의 뉴클레오티드를 갖는 참조 서열과 비교될 수 있다. 서열 동일성 또는 상동성은 널리 공지된 서열 비교 알고리즘, 예컨대 FASTA 생물학적 서열 정렬/비교 소프트웨어 프로그램을 사용하여 결정될 수 있다 (예를 들어, 문헌 [Pearson and Lipman, 1985, 1988] 참조).
관심 유전자 코딩 서열의 부분, 예를 들어 스테레오실린 단백질을 코딩하는 STRC 유전자를 세포로 전달하기 위한 벡터, 플라스미드 등을 포함한 폴리뉴클레오티드가 본원에 제공된다. 일부 실시양태는 19 kb의 29개 엑손을 함유하는 인간 STRC 유전자로부터 유래된 코딩 서열을 제공할 수 있다 (예를 들어, NCBI 진 ID: 161497; AC016135.3; NG_011636.1; NCBI 뉴클레오티드 ID: NM_153700.2; AF375594 참조). 다른 실시양태는 뮤린 (무스 무스쿨루스) STRC 유전자를 제공할 수 있다 (예를 들어, NCBI 진 ID: 140476; AL845466; AF375593; AK144985; NM_080459 참조). 1,809개 아미노산을 갖는 스테레오실린 (STRC) 단백질 또는 STRC 전구체 (예를 들어, NCBI 프로테인 ID: NP_714544; AAL35321; BAE26168; NP_536707; 유니프롯KB/스위스 프롯: Q7RTU9 참조)는 내이 내 외유모 세포의 부동섬모에서 발견되는 큰 세포외 구조 단백질이다.
STRC 유전자 (예를 들어, NCBI 수탁 번호 NG_011636; OMIM # 603720; MIM 606440)는 부동섬모 단부의 적절한 응집 및 위치설정에 중요한 수평 상단 연결자 및 덮개막 연결관과 회합되어 있는, 내이의 외유모 세포의 부동섬모에서 발견되는 큰 세포외 구조 단백질인 스테레오실린 (STRC) 단백질을 코딩한다. STRC 유전자는 염색체 15q15 상에 위치하고, 상염색체 열성 DFNB16 난청 유전자좌를 규정하고, 19 kb를 포괄하는 29개의 엑손을 함유한다. "STRC 폴리뉴클레오티드"는 STRC 폴리펩티드 또는 그의 단편을 코딩하는 핵산 분자를 의미한다.
상염색체 열성 비-증후군성 난청인 DFNB16 청력 상실의 기저 원인은 돌연변이된 STRC 유전자와 연관되었다. 인간 스테레오실린 (STRC) 단백질 (NCBI RefSeq: NP_714544)을 코딩하는 인간 뉴클레오티드 STRC 코딩 서열을 함유하는 인간 STRC 유전자 서열 (유전자 ID: 161497)이며, 신호 서열이 없는 인간 STRC 코딩 서열 (예를 들어, 서열식별번호: 29)은 하기와 같다:
인간 STRC 코딩 서열은 도 2a-2c의 구축물에서 찾아볼 수 있고, 인간 STRC 코딩 서열의 부분은 도 7a-7b 및 도 12a-12b의 구축물에서 찾아볼 수 있다.
인간 STRC 단백질을 코딩하는 인간 mRNA 서열 (NCBI RefSeq: NM153700) (서열식별번호: 30)은 하기와 같다:
스테레오실린 발현은 내이의 감각 유모 세포에서만 발견되었고, 부동섬모, 즉 소리 자극의 기계적감수를 위한 구조를 형성하는 강성 미세융모와 회합된다. 신호 펩티드 서열 (아미노산 1-21에서; 밑줄표시)을 포함하고, 링커 서열 또는 Myc 태그 서열을 포함하지 않으며, 스플라이스 부위가 Ala708과 Cys709 또는 Ala933과 Cys934 (볼드체, 밑줄표시) 사이에 존재할 수 있는 인간 STRC 단백질 (1,775개 아미노산; 서열식별번호: 25)은 하기와 같다:
추정 신호 펩티드 및 여러 소수성 부분을 포함한 1,809개 아미노산을 포함하는 뮤린 STRC 단백질 (NCBI RefSeq: NP_536707)을 코딩하는 뮤린 (무스 무스쿨루스) STRC 유전자 (유전자 ID: 140476; 염기 쌍 79-5508에서의 CDS)이며, 신호 서열이 없는 뮤린 STRC 코딩 서열 (예를 들어, 서열식별번호: 31)은 하기와 같다:
뮤린 STRC 코딩 서열은 도 4a-4d의 구축물에서 찾아볼 수 있고, 뮤린 STRC 코딩 서열의 부분은 도 8a-8b 및 도 13a-13b의 구축물에서 찾아볼 수 있다.
뮤린 STRC 단백질을 코딩하는 뮤린 mRNA 서열 (NCBI RefSeq: NM_080459; 서열식별번호: 32)은 하기와 같다:
신호 펩티드 서열 (아미노산 1-22에서; 밑줄표시)을 포함하고, 링커 서열 또는 Myc 태그 서열을 포함하지 않는 뮤린 STRC 단백질 (1,809개 아미노산; 서열식별번호: 26) (여기서 22개-아미노산 신호 펩티드 서열의 절단은 예측 분자 질량이 194 kD인 1,787개 아미노산을 갖는 단백질을 남김)은 하기 서열을 가지며, 여기서 Ser746 및 Cys747 및 Ala969 및 Cys970 스플라이스 부위는 볼드체, 밑줄표시된 문자이다:
"스테레오실린 (STRC) 단백질"은, 예를 들어 NCBI 수탁 번호 NP_714544 또는 NP_536707; 진뱅크 번호 AAL35321에 대해 적어도 약 80% 아미노산 동일성 (예를 들어, 82%, 85%, 88%, 90%, 95%, 97%, 98%, 99%, 100%)을 갖는 폴리펩티드 또는 그의 단편을 의미한다.
"검출하다"는 검출될 분석물의 존재, 부재 또는 양을 확인하는 것을 지칭한다.
"검출가능한 표지"는 관심 분자에 연결되는 경우에 분광학적, 광화학적, 생화학적, 면역화학적 또는 화학적 수단을 통해 후자의 분자를 검출가능하게 하는 조성물을 의미한다. 예를 들어, 유용한 표지는 방사성 동위원소, 자기 비드, 금속성 비드, 콜로이드성 입자, 형광 염료, 예를 들어 녹색 형광 단백질, 전자-고밀도 시약, 효소 (예를 들어, ELISA에 통상적으로 사용되는 바와 같음), 비오틴, 디곡시게닌 또는 합텐을 포함한다.
"질환"은 세포, 조직 또는 기관의 정상적인 기능을 손상시키거나 방해하는 임의의 상태 또는 장애를 의미한다. 질환의 예는 임의의 병리상태, 예컨대 열성 돌연변이와 연관된 청력 장애, 예를 들어 DFNB16을 포함하나 이에 제한되지는 않는 청력 장애를 포함한다.
"유효량"은 비치료되지 않은 환자에 비해 질환의 증상을 호전시키는 데 요구되는 작용제의 양을 의미한다. 질환의 치유적 치료를 실시하는 데 사용되는 활성 화합물(들)의 유효량은 투여 방식, 대상체의 연령, 체중 및 전반적 건강에 따라 달라진다. 궁극적으로, 담당 의사 또는 수의사는 적절한 양 및 투여 요법을 결정할 것이다. 이러한 양은 "유효량"으로 지칭된다.
"단편"은 폴리펩티드 또는 핵산 서열 또는 분자의 부분을 의미한다. 이러한 부분은 참조 핵산 분자 또는 폴리펩티드의 전체 길이의 적어도 10% 이상 (예를 들어, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 90%)을 함유할 수 있다. 단편은 10개 이상 (예를 들어, 20, 30, 40, 50, 60, 70, 80, 90 또는 100, 200, 300, 400, 500, 600, 700, 800, 900, 1000, 1100, 1200, 1300, 1400, 1500개)의 뉴클레오티드 또는 아미노산을 함유할 수 있다.
"혼성화"는 상보적 핵염기 사이의 왓슨-크릭, 후그스틴 또는 역 후그스틴 수소 결합일 수 있는 수소 결합을 의미한다. 예를 들어, 아데닌 및 티민은 수소 결합의 형성을 통해 쌍형성하는 상보적 핵염기이다.
"동일성"은 관심 서열과 참조 서열 사이의 아미노산 또는 핵산 서열 동일성을 의미한다. "실질적으로 동일한"은 참조 아미노산 서열 (예를 들어, 본원에 기재된 아미노산 서열 중 어느 하나) 또는 핵산 서열 (예를 들어, 본원에 기재된 핵산 서열 중 어느 하나)에 대해 적어도 50% 동일성을 나타내는 폴리펩티드 또는 핵산 분자를 의미한다. 이러한 서열은 비교를 위해 사용된 서열 또는 참조 서열에 대해 아미노산 수준 또는 핵산 수준에서 적어도 60% 이상 (예를 들어, 70%, 75%, 80%, 85%, 90%, 95%, 99%, 100%)의 동일성을 가질 수 있다.
서열 동일성은 서열 분석 소프트웨어 (예를 들어, 제네틱스 컴퓨터 그룹 (53705 위스콘신주 매디슨 유니버시티 애비뉴 1710 소재 유니버시티 오브 위스콘신 바이오테크놀로지 센터)의 서열 분석 소프트웨어 패키지, BLAST, BESTFIT, GAP 또는 PILEUP/PRETTYBOX 프로그램)를 사용하여 측정될 수 있다. 이러한 소프트웨어는 다양한 치환, 결실 및/또는 다른 변형에 상동성 정도를 배정함으로써 동일하거나 유사한 서열을 매칭시킨다. 보존적 치환은 전형적으로 하기 군 내에서의 치환을 포함한다: 글리신, 알라닌; 발린, 이소류신, 류신; 아스파르트산, 글루탐산, 아스파라긴, 글루타민; 세린, 트레오닌; 리신, 아르기닌; 및 페닐알라닌, 티로신. 동일성 정도를 결정하기 위한 예시적인 접근법에서, BLAST 프로그램이 사용될 수 있으며, 여기서 e-3 내지 e-100의 확률 점수는 밀접하게 관련된 서열을 나타낸다.
용어 "단리된", "정제된" 또는 "생물학적으로 순수한"은 그의 천연 상태에서 발견되는 바와 같은 정상적으로 동반되는 성분이 다양한 정도로 없는 물질을 지칭한다. "단리하다"는 원래의 공급원 또는 주변으로부터의 분리 정도를 나타낸다. "정제하다"는 단리보다 더 높은 분리 정도를 나타낸다. "정제된" 또는 "생물학적으로 순수한" 단백질은 임의의 불순물이 단백질의 생물학적 특성에 실질적으로 영향을 미치거나 다른 유해 결과를 유발하지 않도록 다른 물질이 충분히 없다. 즉, 본 개시내용의 핵산 또는 펩티드는 재조합 DNA 기술에 의해 생산되는 경우에 정제되거나 (예를 들어, 세포 물질, 바이러스 물질, 배양 배지가 실질적으로 없음) 또는 화학적으로 합성되는 경우에 화학적 전구체 또는 다른 화학물질이 정제된다. 순도 및 균질성은 전형적으로 분석 화학 기술, 예를 들어 폴리아크릴아미드 겔 전기영동 또는 고성능 액체 크로마토그래피를 사용하여 결정된다. 용어 "정제된"은 핵산 또는 단백질이 전기영동 겔에서 본질적으로 1개의 밴드를 생성함을 나타낼 수 있다. 변형, 예를 들어 인산화 또는 글리코실화에 적용될 수 있는 단백질의 경우, 상이한 변형은 상이한 단리된 단백질을 생성할 수 있으며, 이는 개별적으로 정제될 수 있다.
"단리된 폴리뉴클레오티드"는 본 발명의 핵산 분자가 유래된 유기체의 자연-발생 게놈에서 유전자에 플랭킹된 유전자들이 없는 본 개시내용의 핵산 (예를 들어, DNA)을 의미한다. 따라서, 상기 용어는, 예를 들어 벡터 내로; 자율 복제 플라스미드 또는 바이러스 내로; 또는 원핵생물 또는 진핵생물의 게놈 DNA 내로 혼입되거나; 또는 다른 서열과 독립적으로 별개의 분자 (예를 들어, PCR 또는 제한 엔도뉴클레아제 소화에 의해 생산된 cDNA 또는 게놈 또는 cDNA 단편)로서 존재하는 재조합 DNA를 포함한다. 추가로, 상기 용어는 DNA 분자로부터 전사되는 RNA 분자, 뿐만 아니라 추가의 폴리펩티드 서열을 코딩하는 하이브리드 유전자의 일부인 재조합 DNA를 포함한다.
"단리된 폴리펩티드"는 자연적으로 동반되는 성분들로부터 분리된 본 개시내용의 폴리펩티드를 의미한다. 전형적으로, 폴리펩티드는 자연적으로 회합되는 단백질 및 자연 발생 유기 분자가 적어도 60 중량% 이상 (예를 들어, 75%, 80%, 90%, 95%, 99 중량%) 없는 경우에 단리된 것이다. 본 개시내용의 단리된 폴리펩티드는, 예를 들어 천연 공급원으로부터의 추출에 의해, 이러한 폴리펩티드를 코딩하는 재조합 핵산의 발현에 의해; 또는 단백질을 화학적으로 합성함으로써 수득될 수 있다. 순도는 임의의 적절한 방법, 예를 들어 칼럼 크로마토그래피, 폴리아크릴아미드 겔 전기영동 또는 HPLC 분석에 의해 측정될 수 있다.
"마커"는 질환 또는 장애와 연관된 발현 수준 또는 활성의 변경을 갖는 임의의 단백질 또는 폴리뉴클레오티드를 의미한다.
"기계적감각"은 기계적 자극에 대한 반응을 의미한다. 기계적 자극의 뉴런 신호로의 전환 예의 촉각, 청력 및 균형. 기계적감각 입력은 "기계적전달"이라 불리는 과정을 통해 기계적 자극에 대한 반응으로 전환된다.
본원에 사용된 "작용제를 수득하는"에서와 같은 "수득하는"은 작용제를 합성하거나, 구입하거나 또는 달리 획득하는 것을 포함한다.
본원에 사용된 용어 "예방하다", "예방하는", "예방", "예방적 치료" 등은 장애 또는 상태를 갖지 않지만, 그의 발생 위험이 있거나 또는 그에 걸리기 쉬운 대상체에서 장애 또는 상태가 발생할 확률을 감소시키는 것을 지칭한다.
"프로모터"는 하류 폴리뉴클레오티드의 전사를 지시하기에 충분한 폴리뉴클레오티드를 의미한다. 일부 실시양태에서, 본원에 기재된 폴리뉴클레오티드는 1개 이상의 조절 요소를 포함할 수 있다. 관련 기술분야의 통상의 기술자는 세포, 예를 들어 포유동물 또는 인간 숙주 세포에서 사용하기에 적절한 조절 요소를 선택할 수 있다. 조절 요소의 비제한적 예는 프로모터, 전사 종결 서열, 번역 종결 서열, 인핸서 및 폴리아데닐화 요소를 포함한다. 본원에 기재된 폴리뉴클레오티드는 목적하는 폴리펩티드, 예컨대 스테레오실린을 코딩하는 뉴클레오티드 서열에 작동가능하게 연결된 프로모터 서열을 포함할 수 있다. 본 발명에서 사용하기 위해 고려되는 프로모터는 시토메갈로바이러스 (CMV) 프로모터, SV40 프로모터, 라우스 육종 바이러스 (RSV) 프로모터, 키메라 CMV/닭 β 액틴 프로모터 (CBA) 및 말단절단된 형태의 CBA (smCBA)를 포함하나 이에 제한되지는 않는다. 일부 실시양태에서, 프로모터는 CMV 프로모터이다.
어구 "제약상 허용되는 부형제"는 대상 화합물을 신체의 한 기관 또는 부분으로부터 신체의 또 다른 기관 또는 부분으로 운반 또는 수송하는 데 수반되는 제약상 허용되는 물질, 조성물 또는 비히클, 예컨대 액체 또는 고체 충전제, 희석제, 담체, 용매 또는 캡슐화 물질을 포함할 수 있다. 각각의 담체는 제제의 다른 성분과 상용성이고 환자에게 유해하지 않다는 의미에서 "허용되는" 것이어야 한다. 제약상 허용되는 담체로서의 역할을 할 수 있는 물질의 일부 예는 다음을 포함한다: (1) 당, 예컨대 락토스, 글루코스 및 수크로스; (2) 전분, 예컨대 옥수수 전분 및 감자 전분; (3) 셀룰로스 및 그의 유도체, 예컨대 소듐 카르복시메틸 셀룰로스, 에틸 셀룰로스 및 셀룰로스 아세테이트; (4) 분말화 트라가칸트; (5) 맥아; (6) 젤라틴; (7) 활석; (8) 부형제, 예컨대 코코아 버터 및 좌제 왁스; (9) 오일, 예컨대 땅콩 오일, 목화씨 오일, 홍화 오일, 참깨 오일, 올리브 오일, 옥수수 오일 및 대두 오일; (10) 글리콜, 예컨대 프로필렌 글리콜; (11) 폴리올, 예컨대 글리세린, 소르비톨, 만니톨 및 폴리에틸렌 글리콜; (12) 에스테르, 예컨대 에틸 올레에이트 및 에틸 라우레이트; (13) 한천; (14) 완충제, 예컨대 수산화마그네슘 및 수산화알루미늄; (15) 알긴산; (16) 발열원-무함유 물; (17) 등장성 염수; (18) 링거액; (19) 에틸 알콜; (20) 포스페이트 완충제 용액; 및 (21) 제약 제제에 사용되는 다른 비-독성 상용성 물질.
추가의 적합한 담체 및 그의 제제는, 예를 들어 문헌 [Remington's Pharmaceutical Sciences by E. W. Martin]의 가장 최신판에 기재되어 있다. 투여될 치료제의 양은 투여 방식 및 모드, 연령 및 질환 상태 (예를 들어, 치료 전에 존재하는 청력 상실의 정도)에 따라 달라진다.
"스테레오실린 프로모터"는 유모 다발 내의 인접한 부동섬모의 정단 영역을 연결하는 수평 상단 연결자 및 가장 높은 부동섬모를 위에 놓인 덮개막 (TM)에 부착시키는 연결관과 회합되어 있는, 성숙 와우 내 내유모 세포 (IHC) 또는 외유모 세포 (OHC)에서의 하류 폴리뉴클레오티드의 발현을 지시하기에 충분한 NCBI 참조 서열: NG_011636.1로부터 유래된 조절 폴리뉴클레오티드 서열을 의미한다. 스테레오실린은 또한 전정 유모 세포 및 미성숙 OHC의 운동섬모 주위에서 발현될 수 있다. 본 개시내용의 한 실시양태는 스테레오실린 코딩 서열의 상류의 적어도 350개 이상 (예를 들어, 500, 1000, 2000, 3000, 4000, 5000개)의 염기 쌍을 포함하거나 또는 그로 이루어진 스테레오실린 프로모터를 제공한다.
"감소시키다"는 적어도 5% 이상 (예를 들어, 10%, 15%, 20%, 25%, 50%, 75%, 100%)의 음성 변경을 의미한다.
"참조"는 표준 또는 대조군 조건을 의미한다.
"참조 서열"은 서열 비교를 위한 기초로서 정의되고 사용될 수 있는 서열이다. 참조 서열은 특정한 서열의 부분 또는 전체, 예를 들어 전장 cDNA 또는 유전자 서열의 단편, 또는 완전한 cDNA 또는 유전자 서열일 수 있다. 참조 폴리펩티드 서열의 길이는 폴리펩티드에 대해 적어도 10개 아미노산 이상 (예를 들어, 15, 20, 25, 30, 35, 50, 100개) 또는 그 부근 또는 그 사이의 임의의 정수일 수 있다. 참조 핵산 서열의 길이는 핵산에 대해 적어도 50개 뉴클레오티드 이상 (예를 들어, 55, 60, 75, 90, 100, 200, 300개) 또는 그 부근 또는 그 사이의 임의의 정수일 수 있다.
"특이적으로 결합한다"는 본 개시내용의 폴리펩티드를 인식하고 그에 결합하지만, 자연적으로 본 개시내용의 폴리펩티드를 포함하는 샘플, 예를 들어 생물학적 샘플 내의 다른 분자를 실질적으로 인식하고 그에 결합하지 않는 화합물 또는 항체를 의미한다.
본 개시내용의 방법에 유용한 핵산 분자는 본 개시내용의 폴리펩티드 또는 그의 단편 또는 부분을 코딩하는 임의의 핵산 분자를 포함한다. 이러한 핵산 분자는 내인성 핵산 서열과 100% 동일할 필요는 없지만, 전형적으로 실질적인 동일성을 나타낼 것이다. 내인성 서열에 대해 "실질적 동일성"을 갖는 폴리뉴클레오티드는 전형적으로 이중-가닥 핵산 분자의 적어도 1개의 가닥과 혼성화할 수 있다. 본 발명의 방법에 유용한 핵산 분자는 본 발명의 폴리펩티드 또는 그의 단편을 코딩하는 임의의 핵산 분자를 포함한다. 이러한 핵산 분자는 내인성 핵산 서열과 100% 동일할 필요는 없지만, 전형적으로 실질적인 동일성을 나타낼 것이다. 내인성 서열에 대해 "실질적 동일성"을 갖는 폴리뉴클레오티드는 전형적으로 이중-가닥 핵산 분자의 적어도 1개의 가닥과 혼성화할 수 있다. "혼성화하다"는 다양한 엄격도 조건 하에 상보적 폴리뉴클레오티드 서열 (예를 들어, 본원에 기재된 유전자) 또는 그의 부분 사이에 이중-가닥 분자를 형성하기 위해 쌍을 형성하는 것을 의미한다. (예를 들어, 문헌 [Wahl, G. M. and S. L. Berger (1987) Methods Enzymol. 152:399; Kimmel, A. R. (1987) Methods Enzymol. 152:507] 참조).
혼성화는, 예를 들어 통상적으로 750 mM 미만의 NaCl (예를 들어, 500 mM; 250 mM) 및 75 mM 미만의 시트르산삼나트륨 (예를 들어, 50 mM; 25 mM)일 수 있는 엄격한 염 농도 하에 이루어질 수 있다. 낮은 엄격도 혼성화는 유기 용매, 예를 들어 포름아미드의 부재 하에 수득될 수 있는 반면, 높은 엄격도 혼성화는 적어도 35% 포름아미드 (예를 들어, 50% 포름아미드)의 존재 하에 수득될 수 있다. 엄격한 온도 조건은 통상적으로 적어도 30℃ (예를 들어, 37℃, 42℃)의 온도를 포함할 수 있다. 추가의 파라미터, 예컨대 혼성화 시간, 세제, 예를 들어 소듐 도데실 술페이트 (SDS)의 농도 및 캐리어 DNA의 포함 또는 배제를 변동시키는 것은 관련 기술분야의 통상의 기술자에게 널리 공지되어 있다. 다양한 수준의 엄격도는 필요에 따라 이들 다양한 조건을 조합함으로써 달성될 수 있다. 한 실시양태에서, 혼성화는 30℃에서 750 mM NaCl, 75 mM 시트르산삼나트륨 및 1% SDS 중에서 이루어질 수 있다. 또 다른 실시양태에서, 혼성화는 37℃에서 500 mM NaCl, 50 mM 시트르산삼나트륨, 1% SDS, 35% 포름아미드 및 100 μg/ml 변성 연어 정자 DNA (ssDNA) 중에서 이루어질 수 있다. 추가 실시양태에서, 혼성화는 42℃에서 250 mM NaCl, 25 mM 시트르산삼나트륨, 1% SDS, 50% 포름아미드 및 200 μg/ml ssDNA 중에서 이루어질 수 있다. 이들 조건에 대한 유용한 변동은 관련 기술분야의 통상의 기술자에게 자명할 것이다.
대부분의 적용에 있어서, 혼성화에 이어지는 세척 단계는 또한 엄격도가 달라질 수 있다. 세척 엄격도 조건은 염 농도 및 온도에 의해 정의될 수 있다. 상기와 같이, 세척 엄격도는 염 농도를 감소시킴으로써 또는 온도를 증가시킴으로써 증가될 수 있다. 예를 들어, 세척 단계를 위한 엄격한 염 농도는 30 mM 미만의 NaCl (예를 들어, 15 mM) 및 3 mM 미만의 시트르산삼나트륨 (예를 들어, 1.5 mM)일 수 있다. 세척 단계에 대한 엄격한 온도 조건은 통상적으로 적어도 25℃ (예를 들어, 42℃, 68℃)의 온도를 포함할 수 있다. 또 다른 실시양태에서, 세척 단계는 25℃에서 30 mM NaCl, 3 mM 시트르산삼나트륨 및 0.1% SDS 증에서 이루어질 수 있다. 또 다른 실시양태는 42℃에서 15 mM NaCl, 1.5 mM 시트르산삼나트륨 및 0.1% SDS 중에서 이루어지는 세척 단계를 제공할 수 있다. 추가 실시양태는 68℃에서 15 mM NaCl, 1.5 mM 시트르산삼나트륨 및 0.1% SDS 중에서 이루어지는 세척 단계를 제공할 수 있다. 이들 조건에 대한 추가의 변동은 관련 기술분야의 통상의 기술자에게 자명할 것이다. 혼성화 기술은 관련 기술분야의 통상의 기술자에게 널리 공지되어 있고, 예를 들어 문헌 [Benton and Davis (Science 196:180, 1977); Grunstein and Hogness (Proc. Natl. Acad. Sci., USA 72:3961, 1975); Ausubel et al. (Current Protocols in Molecular Biology, Wiley Interscience, New York, 2001); Berger and Kimmel (Guide to Molecular Cloning Techniques, 1987, Academic Press, New York); 및 Sambrook et al., Molecular Cloning: A Laboratory Manual, Cold Spring Harbor Laboratory Press, New York]에 기재되어 있다.
"대상체"는 인간 또는 비-인간 포유동물, 예컨대 소, 말, 개, 양, 고양이 또는 뮤린을 포함하나 이에 제한되지는 않는 포유동물을 의미한다.
"STRC 단백질 또는 폴리펩티드"는 NCBI 수탁 번호 NP_714544 또는 진뱅크 번호 AAL35321에 대해 적어도 약 85% 이상의 아미노산 서열 동일성을 갖는 폴리펩티드, 또는 청각 기능에 필수적인 STRC를 발현하기에 충분한 활성을 갖는 그의 단편을 의미한다.
본원에 사용된 용어 "치료하다", "치료하는", "치료" 등은 그와 연관된 일부 장애 및/또는 증상의 감소 또는 호전을 지칭한다. 배제되는 것은 아니지만, 장애 또는 상태를 치료하는 것이 장애, 상태 또는 그와 연관된 증상을 완전히 제거하는 것을 요구하지는 않는다는 것이 인지될 것이다.
구체적으로 언급되거나 문맥으로부터 명백하지 않는 한, 본원에 사용된 용어 "또는"은 포괄적인 것으로 이해된다. 구체적으로 언급되거나 문맥으로부터 명백하지 않는 한, 본원에 사용된 단수 용어는 단수 또는 복수인 것으로 이해된다.
본 개시내용에서, "포함한다", "포함하는", "함유하는" 및 "갖는" 등은 미국 특허법에서 그에 부여된 의미를 가질 수 있으며 "포함한다", "포함하는" 등을 의미할 수 있고; "본질적으로 이루어진" 또는 "본질적으로 이루어진다"는 마찬가지로 미국 특허법에서 부여된 의미를 가지며 이 용어는 개방형이어서, 인용된 것의 기초 또는 신규 특징이 인용된 것 초과의 존재에 의해 변화되지 않는 한, 인용된 것 초과의 존재를 허용하지만, 선행 기술 실시양태는 배제한다. "본질적으로 이루어진다"는 것은, 예를 들어 구성성분이 상업적 물질에 존재하는 통상의 불순물과 함께 및 본원에 개시된 실시양태의 작업에 영향을 미치지 않는 수준으로, 예를 들어 5 중량% 미만 또는 1 중량% 미만 또는 심지어 0.5 중량%의 수준으로 존재하는 임의의 다른 첨가제와 함께, 단지 열거된 성분만을 포함하는 것을 의미한다.
본원에 사용된 모든 수치 범위는 종점 및 개시된 값 사이에 개시된 모든 가능한 값을 포함한다. 모든 절반 정수 수치 값의 정확한 값은 또한 구체적으로 개시된 바와 같이 및 개시된 범위의 모든 하위세트에 대한 한계로서 고려된다. 예를 들어, 1 내지 50의 범위는 1, 2, 3, 4, 5, 6, 7, 8, 9, 10, 11, 12, 13, 14, 15, 16, 17, 18, 19, 20, 21, 22, 23, 24, 25, 26, 27, 28, 29, 30, 31, 32, 33, 34, 35, 36, 37, 38, 39, 40, 41, 42, 43, 44, 45, 46, 47, 48, 49 또는 50으로 이루어진 군으로부터의 임의의 수, 수의 조합 또는 하위-범위를 포함하는 것으로 이해된다. 추가적으로, 0.1% 내지 3%의 범위는 구체적으로, 예를 들어 0.1%, 1%, 1.5%, 2.0%, 2.5% 및 3% 또는 그 사이의 임의의 다른 수치 값의 백분율을 개시한다. 추가적으로, 0.1 내지 3%의 범위는 0.5% 내지 2.5%, 1% 내지 3%, 0.1% 내지 2.5% 등을 포함한 원래 범위의 하위세트를 포함한다. 개별 성분의 모든 중량%의 합계는 100%를 초과하지 않을 것으로 이해될 것이다. 본원에 제공된 범위는 범위 내의 모든 값에 대한 약칭인 것으로 이해된다.
본원의 변수의 임의의 정의에서 화학적 기의 목록의 언급은 임의의 단일 기 또는 열거된 기의 조합으로서의 그 변수의 정의를 포함한다. 본원의 변수 또는 측면에 대한 실시양태의 언급은 임의의 단일 실시양태로서의 또는 임의의 다른 실시양태 또는 그의 부분과 조합된 그 실시양태를 포함한다.
본원에 제공된 임의의 조성물 또는 방법은 본원에 제공된 임의의 다른 조성물 및 방법 중 하나 이상과 조합될 수 있다.
본 개시내용은 시스템 (예를 들어, 벡터, 재조합 바이러스), 분할 관심 단백질, 예컨대 STRC 단백질을 코딩하는 핵산 서열 또는 구축물, 및 본원에 기재된 핵산 서열 또는 구축물을 사용하여 관심 단백질 (예를 들어, STRC)을 숙주, 숙주 세포 또는 세포 내로 전달하는 방법에 관한 것이다. 단백질의 아미노 말단 (N-말단) 단편 및 단백질의 카르복시 말단 (C-말단) 단편을 포함하는 분할 단백질은, 예를 들어 벡터 (예를 들어, 바이러스 벡터, 예컨대 아데노-연관 바이러스 (AAV) 또는 렌티바이러스)를 사용하는 세포 내로의 전달을 위해 상이한 및 별개의 핵산 서열 또는 구축물 상에 각각 코딩된다. 관심 단백질의 N-말단 및 C-말단 폴리펩티드 단편은, 예를 들어 인테인-매개 단백질 스플라이싱을 사용하여 함께 연결되어 전장 관심 단백질을 형성할 수 있으며, 여기서 관심 단백질의 N-말단 및 C-말단 폴리펩티드 단편은 펩티드 결합에 의해 연결된다. 상이한 종들 사이의 분할 부위는 유사하거나 상동인 영역에 위치할 것이다.
벡터 시스템
일부 실시양태는 목적하는 유전자 구축물을 함유하는 적어도 1개의 벡터를 포함하는, 목적하는 전장 단백질의 코딩 서열을 전달하기 위한 벡터 (예를 들어, 캡시드, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈, 렌티바이러스) 시스템을 제공할 수 있다. 도 1은 이러한 예시적인 AAV STRC 구축물의 개략적 표현을 보여준다. 다른 실시양태에서, 벡터 시스템은 전체 인간 STRC 코딩 서열 (서열식별번호: 1)을 포함할 수 있으며, 여기서 5' 말단에서의 뉴클레오티드 서열 (도 2a-2c; 서열식별번호: 33)은 "ATG" 개시 코돈 (볼드체)으로 시작하고 정지 코돈 (대문자, 이탤릭체 및 밑줄표시)으로 끝나며, 신호 펩티드 코딩 서열 (소문자, 이탤릭체 및 밑줄표시; 서열식별번호: 9)은 STRC 코딩 서열의 상류에 위치한다. 임의로, 3' 말단에 링커 서열 (볼드체 및 이탤릭체; 서열식별번호: 34) 및 myc 태그를 코딩하는 서열 (소문자; 서열식별번호: 35)이 포함될 수 있으며, 이는 단백질 단리 (예를 들어, 웨스턴 블롯팅, 면역형광, 면역침전)를 포함하나 이에 제한되지는 않는 후속 연구에 사용될 수 있다. 도 3은 도 2의 인간 STRC 뉴클레오티드 서열에 의해 코딩되는 아미노산 서열 (서열식별번호: 36)을 제시하며, 인간 STRC 단백질 서열은 ATG 코돈에 의해 코딩되는 메티오닌 (M) (볼드체), 신호 펩티드 서열 (소문자, 이탤릭체 및 밑줄표시; 서열식별번호: 10), 임의적인 링커 서열 (볼드체 및 이탤릭체) (N-term-TRTRPL-C-term; 서열식별번호: 37) 및 임의적인 Myc 태그 (소문자; 서열식별번호: 27)를 포함한다.
다른 실시양태에서, 벡터 시스템은 전체 뮤린 STRC 코딩 서열 (서열식별번호: 3)을 포함할 수 있으며, 여기서 5' 말단에서의 뉴클레오티드 서열 (도 4a-4d; 서열식별번호: 38)은 "ATG" 개시 코돈 (볼드체)으로 시작하고 정지 코돈 (대문자, 이탤릭체 및 밑줄표시)으로 끝나며, 신호 펩티드 코딩 서열 (소문자, 이탤릭체 및 밑줄표시; 서열식별번호: 11)은 STRC 코딩 서열의 상류에 위치한다. 임의로, 3' 말단에 링커 서열 (볼드체 및 이탤릭체; 서열식별번호: 34) 및 myc 태그를 코딩하는 서열 (소문자; 서열식별번호: 35)이 포함될 수 있으며, 이는 단백질 단리 (예를 들어, 웨스턴 블롯팅, 면역형광, 면역침전)를 포함하나 이에 제한되지는 않는 후속 연구에 사용될 수 있다. 도 5는 도 4의 뮤린 STRC 뉴클레오티드 서열에 의해 코딩되는 아미노산 서열을 제시하며, 뮤린 STRC 단백질 서열 (서열식별번호: 39)은 ATG 코돈에 의해 코딩되는 메티오닌 (M) (볼드체), 신호 펩티드 서열 (소문자, 이탤릭체 및 밑줄표시), 임의적인 링커 서열 (볼드체 및 이탤릭체) (서열식별번호: 37) 및 임의적인 Myc 태그 (소문자) (서열식별번호: 27)를 포함한다.
관련 기술분야의 통상의 기술자는 문헌 [MR Green and J Sambrook, Molecular Cloning: A Laboratory Manual (2012), 4th Ed.; Ausubel et al., Current Protocols in Molecular Biology (2003)] (이들 둘 다는 본원에 참조로 포함됨)에 기재된 표준 재조합 기술을 통해 벡터 (예를 들어, 바이러스 (박테리오파지, 동물 바이러스 및 식물 바이러스, 캡시드), 플라스미드, 코스미드 및 인공 염색체 (예를 들어, YAC) 포함)를 구축하기에 충분히 준비가 갖추어져 있을 것으로 이해된다. 추가적으로, DNA를 세포로 도입 또는 전달하는 방법은, 예를 들어 문헌 [Sung, Y., Kim, S. "Recent advances in the development of gene delivery systems." Biomater Res 23, 8 (2019); Jin, Lian et al. "Current progress in gene delivery technology based on chemical methods and nano-carriers." Theranostics 4(3):240-255, 2014; Nayerossadat N, Maedeh T, Ali PA. "Viral and nonviral delivery systems for gene delivery." Adv Biomed Res. 1:27, 2012; Machida, Curtis A. Viral Vectors for Gene Therapy Methods and Protocols. Humana Press, 2003; Heiser, William C. Gene Delivery to Mammalian Cells. Humana Press, 2004] (이들은 각각 본원에 참조로 포함됨)에 개시되어 있다.
인테인-매개 단백질 트랜스-스플라이싱
다른 실시양태는 인테인을 사용하여 동일한 목적하는 관심 단백질의 상이한 부분을 각각 전달하기 위한 2개의 벡터를 포함하는 이중-벡터 시스템을 포함하는 벡터 시스템을 제공할 수 있다. 인테인은 단백질 인트론인 것으로 간주될 수 있으며, 여기서 이들은 아미노산 서열로부터 그 자체를 절제하고 남아있는 플랭킹 영역 (엑스테인)을 단백질 스플라이싱으로 공지된 과정에 의해 펩티드 결합과 연결시킬 수 있는 단백질의 일부이다. 예를 들어, 문헌 [Mills et al. "Protein Splicing: How Inteins Escape from Precursor Proteins" JBC. 289(21):14498-14505, 2014]을 참조하며, 이는 인테인-매개 단백질 트랜스-스플라이싱 과정에 대해 그 전문이 본원에 참조로 포함된다. 인테인-매개 단백질 스플라이싱은 인테인을 함유하는 mRNA가 단백질로 번역된 후에 발생한다. 도 6을 참조한다.
인테인은 숙주 단백질-인테인 융합체로부터 그 자체를 절제하는 반응을 촉매하여, 성숙 숙주 단백질 (엑스테인) 및 분리된 인테인을 생성하는 효소의 부류이며, 여기서 펩티드 결합은 공여자 인테인과 수용자 인테인 사이의 스플라이스 접합부를 라이게이션한다. 문헌 [Perler, F.B. (InBase. The intein database. Nucleic Acids Res. 30:383-384, 2002)] (이들 모두는 그 전문이 본원에 참조로 포함될 수 있음)에 의해 확인된 것 (예를 들어, 노스톡 푼크티포르메(Nostoc punctiforme) PCC 73102 (ATCC® 29133™)로부터의 Npu-PCC73102 (DnaE-c 인테인 (수탁 번호 ZP_00108882); DnaE-n 인테인 (수탁 번호 ZP_00111398)) (이들 모두는 그 전문이 본원에 참조로 포함될 수 있음)을 포함하나 이에 제한되지는 않는 임의의 공지된 인테인이 본 개시내용의 실시양태에 사용될 수 있다.
본 개시내용의 일부 실시양태에서, 시아노박테리아 노스톡 푼크티포르메 (Npu)로부터의 DNA 폴리머라제 III DnaE의 촉매 서브유닛이 본원에 기재된 스플릿-인테인-STRC 이중-벡터 시스템에 사용될 수 있다. 예를 들어, 시아노박테리아 노스톡 푼크티포르메 (Npu)로부터의 DNA 폴리머라제 III dnaE의 알파 서브유닛이 존재하며, 이는 자연적으로 분할되고 2개의 유전자 dnaE-n 및 dnaE-c에 위치한다. dnaE의 N- 및 C-말단 부분은 게놈 내 및 반대편 DNA 가닥 상의 2개의 별개의 유전자에 의해 코딩된다. dnaE-n 코딩되는 단백질은 아미노-말단 (N-말단) dnaE 단편 (예를 들어, N-엑스테인) 및 아미노 말단 인테인 (N-인테인)을 함유하는 반면, dnaE-c는 카르복시-말단 인테인 (C-인테인) 엔티티가 선행하는 카르복시-말단 (C-말단) dnaE 단편 (예를 들어, C-엑스테인)을 함유하는 단백질을 코딩한다. N-인테인 및 C-인테인은 서로 인식하고, 아미노산 서열로부터 그 자체를 스플라이싱하며, 동시에 펩티드 결합을 통해 관심 플랭킹 N- 및 C-말단 엑스테인을 라이게이션 또는 융합시켜, 융합체를 생성함으로써 전장 관심 단백질을 형성한다.
인테인 활성은 콘텍스트 의존성일 수 있으며, 라이게이션 또는 융합 접합부 주위의 특정 펩티드 서열 (N- 및 C-엑스테인으로 불림)이 효율적인 스플라이싱이 일어나는 데 요구될 수 있다. 예를 들어, C-엑스테인 내의 제1 잔기로서 티올 또는 히드록실 기 (예를 들어, 시스테인 (Cys), 세린 (Ser), 트레오닌 (Thr))를 함유하는 아미노산이 효율적인 스플라이싱에 유용할 수 있다. 천연 시스테인은 스플라이스 부위로서 사용될 수 있다. 예를 들어, AAV 벡터는, 예를 들어 서열식별번호: 26의 위치 747 (Cys747; 변이체 1 & 3) 및 970 (Cys970; 변이체 2 & 4)에서 천연 시스테인을 이용할 수 있고, 이는 Ser746과 Cys747 또는 Ala969와 Cys970 사이의 스플라이스 부위를 제공할 수 있으며 (도 31a-31b), 여기서 분할 부위는 아미노산 서열: ELLS C FSPV (서열식별번호: 60) 또는 GPLA C FLSP (서열식별번호: 61) 또는 그의 부분에서 발생할 수 있다. 또 다른 예는 서열식별번호: 25의 Ala708과 Cys709 또는 Ala933과 Cys934 사이의 스플라이스 부위를 제공하며, 여기서 분할 부위는 아미노산 서열: ELLA C FSPV (서열식별번호: 62) 또는 GPLACFLSP (서열식별번호: 63) 또는 그의 부분에서 발생할 수 있다.
본 개시내용의 한 실시양태는 관심 단백질, 예를 들어 스테레오실린의 각각의 절반을 갖는 엑스테인 영역을 제공한다. 예를 들어, 엑스테인 영역은 N-말단 스테레오실린 및 C-말단 스테레오실린을 포함할 수 있고, 이는 펩티드 결합을 통해 융합되는 경우에 전장 스테레오실린을 구성한다 (예를 들어, NCBI: NM_153700; NP_714544; NM_080459; NP_536707; 진뱅크: BK000138; AF375594; DAA00085; AF375593; AAL35321). 도 6을 참조한다. 또 다른 실시양태는 관심 단백질 (예를 들어, 스테레오실린)의 N-말단 부분 및 C-말단 부분의 합계가 100%인, 스테레오실린에 대한 상이한 분할-부위를 제공한다. 추가 실시양태에서, 분할 부위는 단백질 2차 구조의 나선 (예를 들어, 알파) 내에, 그 후에, 그 전에 또는 그에 인접하여 발생할 수 있다. 한 실시양태는 베타 가닥 또는 가교 내에 있지 않은 분할 부위를 제공할 수 있다. 또 다른 실시양태는 코일 영역의 바로 상류의 나선 (예를 들어, 알파) 내의 분할 부위를 제공한다. 또 다른 실시양태는 관심 단백질 (예를 들어, 스테레오실린) 및 막횡단 도메인의 외부의, 즉 막횡단 부분이 아닌 관심 단백질의 단편을 제공한다.
예를 들어, 분할은 관심 단백질의 N-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 15 또는 뮤린 서열식별번호: 16)이 전장 관심 단백질 (예를 들어, 전장 인간 서열식별번호: 2 또는 서열식별번호: 25 또는 뮤린 서열식별번호: 4 또는 서열식별번호: 26)의 N-말단 단부의 적어도 10% 이상 (예를 들어, 15%, 20%, 25%, 30%, 40%, 45%, 50%, 55%, 60%, 65%, 70%, 75%, 80%, 85%, 90%, 95%, 100%)의 길이를 포함하도록 이루어질 수 있다. 추가 실시양태는 전장 관심 단백질 (예를 들어, 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 N-말단 단부의 100% 이하 (예를 들어, 99%, 97%, 95%, 90%, 85%, 80%, 75%, 70%, 65%, 60%, 55%, 50%, 45%, 40%, 35%, 30%, 25%, 20%, 15%, 10%)의 길이를 포함하는 관심 단백질의 N-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 15 또는 뮤린 서열식별번호: 16)을 제공한다. 하나의 다른 실시양태는 전장 관심 단백질 (예를 들어, 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 N-말단 단부의 10% - 100% (예를 들어, 15%-90%, 20%-80%, 30%-70%, 40%-60%, 50%)의 길이를 포함하는 관심 단백질의 N-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 15 또는 뮤린 서열식별번호: 16)을 제공할 수 있다. 추가 실시양태는 전장 관심 단백질 (예를 들어, 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 N-말단 단부의 54% 미만 (예를 들어, 53%, 52%, 51%, 50%, 45%, 43%, 41%, 40%) 및/또는 그에 대해 54% 미만의 동일성 및/또는 그의 54% 미만의 길이의 관심 단백질의 N-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 15 또는 뮤린 서열식별번호: 16)을 제공한다. 추가 실시양태는 전장 관심 단백질 (예를 들어, 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 N-말단 단부의 54% 미만인 길이를 포함하는 관심 단백질의 N-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 15 또는 뮤린 서열식별번호: 16)에 관한 것일 수 있다. 또 다른 실시양태는 전장 관심 단백질 (예를 들어, 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 N-말단 단부의 40% 이상 (예를 들어, 41%, 42%, 43%, 44%, 45%, 50%, 51%, 52%, 53%) 및/또는 그에 대해 적어도 41% 이상의 동일성 및/또는 그의 41% 이상의 길이를 포함하는 관심 단백질의 N-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 15 또는 뮤린 서열식별번호: 16)을 제공한다.
또 다른 실시양태에서, 관심 단백질의 C-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 23 또는 뮤린 서열식별번호: 24)은 전장 관심 단백질 (예를 들어, 스테레오실린; 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 C-말단 단부의 적어도 10% 이상 (예를 들어, 15%, 20%, 25%, 30%, 40%, 50%, 60%, 70%, 80%, 90%; 100%)의 길이를 포함한다. 추가 실시양태는 전장 관심 단백질 (예를 들어, 스테레오실린; 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 C-말단 단부의 100% 이하 (예를 들어, 99%, 97%, 95%, 90%, 85%, 80%, 75%, 70%, 65%, 60%, 55%, 50%, 45%, 40%, 35%, 30%, 25%, 20%, 15%, 10%)의 길이를 포함하는 관심 단백질의 C-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 23 또는 뮤린 서열식별번호: 24)을 제공한다. 하나의 다른 실시양태는 전장 관심 단백질 (예를 들어, 스테레오실린; 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 C-말단 단부의 10% - 99% (예를 들어, 15%-90%, 20%-80%, 30%-70%, 40%-60%, 50%)의 길이를 포함하는 관심 단백질의 C-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 23 또는 뮤린 서열식별번호: 24)을 제공할 수 있다. 추가 실시양태는 전장 관심 단백질 (예를 들어, 스테레오실린; 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 C-말단 단부의 46% 이상을 포함하는 관심 단백질의 C-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 23 또는 뮤린 서열식별번호: 24)을 제공한다. 추가 실시양태는 전장 관심 단백질 (예를 들어, 스테레오실린; 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 C-말단 단부의 46% 이상 (예를 들어, 47%, 48%, 49%, 50%, 55%, 60%)인 길이 및/또는 그에 대해 46% 이상의 동일성 및/또는 그의 46% 이상의 길이를 포함하는 관심 단백질의 C-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 23 또는 뮤린 서열식별번호: 24)에 관한 것일 수 있다. 추가 실시양태는 전장 관심 단백질 (예를 들어, 스테레오실린; 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 N-말단 단부의 46% 이상 (예를 들어, 47%, 48%, 49%, 50%, 55%, 60%)인 길이를 포함하는 관심 단백질의 C-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 23 또는 뮤린 서열식별번호: 24)에 관한 것일 수 있다. 또 다른 실시양태는 전장 관심 단백질 (예를 들어, 스테레오실린; 전장 인간 서열식별번호: 25 또는 뮤린 서열식별번호: 26)의 C-말단 단부의 60% 이하 (예를 들어, 59%, 58%, 57%, 56%, 55%, 50%, 45%) 및/또는 그에 대해 60% 이하의 동일성 및/또는 그의 60% 이하의 길이를 포함하는 관심 단백질의 C-말단 부분 (예를 들어, 스테레오실린; 인간 서열식별번호: 23 또는 뮤린 서열식별번호: 24)을 제공한다.
추가 실시양태는, 예를 들어 스테레오실린의 N-말단 및 C-말단 단편을 형성하기 위한, 인간 서열식별번호: 25의 Ala708과 Cys709 또는 Ala933과 Cys934 사이의 전장 야생형 스테레오실린 단백질의 분할, 또는 뮤린 서열식별번호: 26의 Ser746과 Cys747 또는 Ala969와 Cys970 사이의 분할을 제공할 수 있다.
이중-벡터 시스템
본 개시내용의 한 실시양태는 세포에서 관심 단백질을 발현시키기 위한 이중-벡터 시스템을 제공하며, 여기서 이중-벡터 시스템은 하기를 포함한다:
a) 5'에서 3' 방향으로:
- 부분 코딩 서열의 5'-말단에 있는 신호 서열 (예를 들어, 서열식별번호: 11; 서열식별번호: 12를 코딩함);
- 관심 단백질의 아미노 말단 (N-말단) 부분 (예를 들어, STRC; 서열식별번호: 15; 서열식별번호: 16)을 코딩하는 부분 코딩 서열;
- 스플라이스 공여자 서열을 코딩하는 서열 (예를 들어, 인테인의 아미노 말단 단편 (N-인테인); 서열식별번호: 13; 서열식별번호: 14를 코딩함)
을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터 (예를 들어, 캡시드, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈, 렌티바이러스); 및
b) 5'에서 3' 방향으로:
- 스플라이스 수용자 서열의 상류일 수 있는 신호 서열 (예를 들어, 서열식별번호: 11; 서열식별번호: 12를 코딩함);
- 스플라이스 수용자 서열을 코딩하는 서열 (예를 들어, 인테인의 카르복시 말단 단편 (C-인테인); 서열식별번호: 21; 서열식별번호: 22를 코딩함);
- 관심 단백질의 카르복시 말단 (C-말단) 부분 (예를 들어, STRC; 서열식별번호: 23; 서열식별번호: 24)을 코딩하는 부분 코딩 서열
을 포함하는 제2 뉴클레오티드 서열을 포함하는 제2 벡터 (예를 들어, 캡시드, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈, 렌티바이러스).
추가 실시양태는 세포에서 관심 단백질을 발현시키기 위한 이중-벡터 시스템을 제공하며, 여기서 이중-벡터 시스템은 하기를 포함한다 (예를 들어, 도 6 참조):
a) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열 (예를 들어, 서열식별번호: 11; 서열식별번호: 12를 코딩함);
- 관심 단백질의 아미노 말단 (N-말단) 부분 (예를 들어, STRC; 서열식별번호: 15; 서열식별번호: 16)을 코딩하는 부분 코딩 서열인, 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 부분 코딩 서열;
- 스플라이스 공여자 서열을 코딩하는 서열 (예를 들어, 인테인의 아미노 말단 단편 (N-인테인); 서열식별번호: 13; 서열식별번호: 14를 코딩함)인, 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 스플라이스 공여자 서열 (예를 들어, N-인테인을 코딩함);
- 폴리-아데닐화 (폴리A) 신호 서열;
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터; 및
b) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열 (예를 들어, 서열식별번호: 11; 서열식별번호: 12를 코딩함);
- 스플라이스 수용자 서열을 코딩하는 서열 (예를 들어, 인테인의 카르복시 말단 단편 (C-인테인); 서열식별번호: 21; 서열식별번호: 22를 코딩함)인, 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 스플라이스 수용자 서열 (예를 들어, C-인테인을 코딩함);
- 관심 단백질의 카르복시 말단 (C-말단) 부분 (예를 들어, STRC; 서열식별번호: 23; 서열식별번호: 24)을 코딩하는 부분 코딩 서열인, 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 부분 코딩 서열;
- 폴리-아데닐화 (폴리A) 신호 서열;
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제2 뉴클레오티드 서열을 포함하는 제2 벡터.
또 다른 실시양태는 제1 벡터가 5'에서 3' 방향으로 서열식별번호: 5 또는 7의 서열을 포함하는 제1 뉴클레오티드 서열을 포함할 수 있는 이중-벡터 시스템에 관한 것일 수 있다. 예를 들어, 도 7a, 도 7b, 도 8a, 도 8b 및 도 9를 참조한다. 도 7a-7b (서열식별번호: 5) 및 도 8a-8b (서열식별번호: 7)는 5'에서 3' 방향으로 개시 코돈 (ATG, 볼드체), 신호 서열 (이탤릭체, 밑줄표시) (신호 서열: 5'-GCTCTCAGCCTCTGGCCCCTGCTGCTGCTGCTGCTGCTGCTGCTGCTGCTGTCCTTTGCA-3'; 서열식별번호: 40; 5'-GCTCTGAGCCTCCAGCCCCAGCTGCTCCTTCTCCTGTCGCTCCTGCCGCAGGAAGTGACTTCA-3'; 서열식별번호: 41), STRC 유전자의 N-말단 부분의 코딩 서열 (흑색) 및 N-인테인 (밑줄표시) (N-인테인 서열: 5'-TGCCTGTCATACGAAACCGAGATACTGACAGTAGAATATGGCCTTCTGCCAATCGGGAAGATTGTGGAGAAACGGATAGAATGCACAGTTTACTCTGTCGATAACAATGGTAACATTTATACTCAGCCAGTTGCCCAGTGGCACGACCGGGGAGAGCAGGAAGTATTCGAATACTGTCTGGAGGATGGAAGTCTCATTAGGGCCACTAAGGACCACAAATTTATGACAGTCGATGGCCAGATGCTGCCTATAGACGAAATCTTTGAGCGAGAGTTGGACCTCATGCGAGTTGACAACCTTCCTAATTAATAG-3'; 서열식별번호: 42)을 포함하는 뉴클레오티드 서열을 도시하며, 여기서 코딩 서열은 스테레오실린 (STRC) 단백질을 코딩한다. 도 9는 ITR, 프로모터 및 폴리A 테일을 포함한 추가의 요소를 보여주며, 여기서 뮤린 5'-STRC는 전장 스테레오실린 (STRC) 단백질의 N-말단 부분 (1-746 (Ser) 아미노산; 79.7 kDa)을 코딩한다. 도 10 및 11은 제1 뉴클레오티드 서열에 의해 코딩되는 아미노산 서열을 보여주며, 여기서 STRC 단백질의 N-말단 부분을 함유하는 아미노산 서열 (각각 서열식별번호: 6; 서열식별번호: 8)은 ATG 코돈에 의해 코딩되는 메티오닌 (M) (볼드체), 신호 펩티드 서열 (소문자, 이탤릭체, 밑줄표시) (신호 펩티드 서열: N-ALSLWPLLLLLLLLLLLSFA-C; 서열식별번호: 43; N-ALSLQPQLLLLLSLLPQEVTS-C; 서열식별번호: 44), 스테레오실린 단백질의 N-말단 부분 (흑색) 및 N-인테인 (볼드체, 밑줄표시) (N-CLSYETEILTVEYGLLPIGKIVEKRIECTVYSVDNNGNIYTQPVAQWHDRGEQEVFEYCLEDGSLIRATKDHKFMTVDGQMLPIDEIFERELDLMRVDNLPN-C; 서열식별번호: 45)을 포함한다.
추가 실시양태는 이중-벡터 시스템을 제공할 수 있으며, 여기서 제2 벡터는 5'에서 3' 방향으로 서열식별번호: 17 또는 19의 서열을 포함하는 제2 뉴클레오티드 서열을 포함할 수 있다. 예를 들어, 도 12a, 도 12b, 도 13a, 도 13b 및 도 14를 참조한다. 도 12a-12b (서열식별번호: 17) 및 도 13a-13b (서열식별번호: 19)는 5'에서 3' 방향으로, 개시 코돈 (볼드체 ATG), 신호 서열 (소문자, 이탤릭체 및 밑줄표시; 각각 서열식별번호: 9; 서열식별번호: 11), C-인테인 서열 (볼드체 및 밑줄표시) (5'-ATCAAGATAGCTACAAGGAAGTATCTTGGCAAACAAAACGTTTATGATATTGGAGTCGAAAGAGATCACAACTTTGCTCTGAAGAACGGATTCATAGCTTCTAAT-3'; 서열식별번호: 46), STRC 유전자의 C-말단 부분의 코딩 서열 (흑색) (여기서 코딩 서열은 스테레오실린 (STRC) 단백질을 코딩함), 링커 서열 (볼드체 및 이탤릭체) (5'-ACGCGTACGCGGCCGCTC-3'; 서열식별번호: 47) 및 Myc 태그 서열 (소문자) (5'-GAGCAGAAACTCATCTCAGAAGAGGATCTGTAATAG-3'; 서열식별번호: 48) 및 정지 코돈 (이탤릭체 및 밑줄표시)을 포함하는 뉴클레오티드 서열을 도시한다. 도 14는 ITR, 프로모터 및 폴리A 테일을 포함한 추가의 요소를 보여주며, 여기서 뮤린 3'-STRC는 전장 스테레오실린 (STRC) 단백질의 C-말단 부분 (747 (Cys)-1,810 아미노산; 116.7 kDa)을 코딩한다. 도 15 및 16은 제2 뉴클레오티드 서열에 의해 코딩되는 아미노산 서열을 보여주며, 여기서 C-말단 부분의 아미노산 서열 (서열식별번호: 18; 서열식별번호: 20)은 ATG 코돈에 의해 코딩되는 메티오닌 (M) (볼드체), 신호 펩티드 서열 (소문자, 이탤릭체 및 밑줄표시) (서열식별번호: 10; 서열식별번호: 44), C-인테인 (볼드체 및 밑줄표시) (N-IKIATRKYLGKQNVYDIGVERDHNFALKNGFIASN-C; 서열식별번호: 49), 스테레오실린 단백질의 C-말단 부분 (흑색), 링커 서열 (볼드체 및 이탤릭체) (N-TRTRPL-C; 서열식별번호: 50) 및 Myc 태그 (소문자) (서열식별번호: 27)를 포함한다. 한 실시양태는 스테레오실린 단백질의 C-말단 부분이 시스테인 (C; Cys), 페닐알라닌 (F; Phe) 및 세린 (S; Ser)으로 시작되는 전장 STRC 단백질을 제공할 수 있다 (도 17).
추가 실시양태에서, 이중-벡터 시스템은 5'에서 3' 방향으로 서열식별번호: 51의 서열을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터를 제공하지 않을 수 있다. 예를 들어, 도 18a, 도 18b 및 도 19를 참조한다. 도 18a-18b (서열식별번호: 51)는 5'에서 3' 방향으로, 개시 코돈 (ATG, 볼드체), 신호 서열 (소문자, 이탤릭체 및 밑줄표시) (서열식별번호: 11), STRC 유전자의 N-말단 부분의 코딩 서열 (흑색) 및 N-인테인 (볼드체 및 밑줄표시) (서열식별번호: 42) (여기서 코딩 서열은 스테레오실린 (STRC) 단백질을 코딩함) 및 정지 코돈 (이탤릭체 및 밑줄표시)을 포함하는 뉴클레오티드 서열을 도시한다. 도 19는 ITR, 프로모터 및 폴리A 테일을 포함한 추가의 요소를 보여주며, 여기서 5'-STRC는 전장 스테레오실린 (STRC) 단백질의 N-말단 부분 (1-969 (Ala) 아미노산; 104.8 kDa)을 코딩한다. 도 20은 제1 뉴클레오티드 서열에 의해 코딩되는 아미노산 서열을 보여주며, 여기서 N-말단 부분의 아미노산 서열 (서열식별번호: 52)은 ATG 코돈에 의해 코딩되는 메티오닌 (M) (볼드체), 신호 펩티드 서열 (소문자, 이탤릭체 및 밑줄표시) (서열식별번호: 44), 스테레오실린 단백질의 N-말단 부분 (흑색) 및 N-인테인 (볼드체 및 밑줄표시) (서열식별번호: 45)을 포함한다.
추가 실시양태는 5'에서 3' 방향으로 서열식별번호: 53의 서열을 포함하는 제2 뉴클레오티드 서열을 포함하는 제2 벡터를 갖는 이중-벡터 시스템을 제공하지 않을 수 있다. 예를 들어, 도 21a, 도 21b 및 도 22를 참조한다. 도 21a-21b (서열식별번호: 53)는 5'에서 3' 방향으로, 개시 코돈 (볼드체 ATG), 신호 서열 (소문자, 이탤릭체 및 밑줄표시) (서열식별번호: 11), C-인테인 서열 (볼드체 및 밑줄표시) (서열식별번호: 21), STRC 유전자의 C-말단 부분의 코딩 서열 (흑색) (여기서 코딩 서열은 스테레오실린 (STRC) 단백질을 코딩함), 링커 서열 (볼드체 및 이탤릭체) (서열식별번호: 47), Myc 태그 서열 (소문자) (서열식별번호: 48) 및 정지 코돈 (이탤릭체 및 밑줄표시)을 포함하는 뉴클레오티드 서열을 도시한다. 도 22는 ITR, 프로모터 및 폴리A 테일을 포함한 추가의 요소를 보여주며, 여기서 3'-STRC는 전장 스테레오실린 (STRC) 단백질의 C-말단 부분 (970 (Cys)-1,810 아미노산; 91.6 kDa)을 코딩한다. 도 23은 제2 뉴클레오티드 서열에 의해 코딩되는 아미노산 서열을 보여주며, 여기서 C-말단 부분의 아미노산 서열 (서열식별번호: 54)은 ATG 코돈에 의해 코딩되는 메티오닌 (M) (볼드체), 신호 펩티드 서열 (소문자, 이탤릭체 및 밑줄표시) (서열식별번호: 44), C-인테인 (볼드체 및 밑줄표시) (서열식별번호: 49), 스테레오실린 단백질의 C-말단 부분 (흑색), 링커 서열 (볼드체 및 이탤릭체) (서열식별번호: 50) 및 Myc 태그 (소문자) (서열식별번호: 27)를 포함한다.
이중-벡터 시스템의 한 실시양태는 관심 단백질 (예를 들어, 스테레오실린)의 각각의 분할된 부분, 즉 N-말단 부분 및 C-말단 부분에 대한 벡터를 제공한다. 관심 단백질 (예를 들어, 스테레오실린)의 분할된 부분 및 관심 단백질을 조절, 생산 또는 발현시키는 데 필요한 임의의 추가의 영역은 각각의 부분 및 연관된 영역이 그의 각각의 벡터 (예를 들어, 바이러스 (예를 들어, 바이러스 벡터, 박테리오파지, 파지, 레트로바이러스), 플라스미드, 코스미드, 박테리아 인공 염색체, 효모 인공 염색체, 인간 인공 염색체)의 적재 용량을 초과하지 않도록 하는 것이다. 동일한 관심 단백질의 분할된 부분 및 추가의 영역은 선택된 벡터의 적재 용량을 초과하는 크기여서는 안된다.
본 개시내용의 한 실시양태는 4 kB 이상 (예를 들어, 4.5 kB, 5 kB, 5.5 kB, 5.8 kB, 6 kB, 6.5 kB, 7 kB, 7.5 kB, 8 kB, 8.5 kB, 9 kB, 9.5 kB, 10 kB, 11 kB, 12 kB)을 포함한 큰 코딩 서열을 갖는 유전자를 전달하기 위한 벡터 시스템 (예를 들어, 이중-벡터 시스템)을 제공한다. 본 개시내용의 벡터 (예를 들어, 제1 벡터 및 제2 벡터)는 각각 바이러스 벡터 (예를 들어, 아데노바이러스, 아데노-연관 바이러스 (AAV), 렌티바이러스, 단순 포진 바이러스 I, 백시니아 바이러스)일 수 있고, 일부 실시양태에서, 바이러스 벡터는 AAV 벡터 또는 재조합 AAV 벡터일 수 있다. 또 다른 실시양태는 동일하거나 상이한 혈청형 (예를 들어, AAV1, AAV2, AAV3, AAV4, AAV5, AAV6, AAV7, AAV8, AAV9, AAV10, AAV11, 합성 혈청형)의 바이러스 벡터를 제공할 수 있다. 본원에 기재된 개시내용에 유용한 AAV 혈청형은 AAV1, AAV2, AAV5, AAV6, AAV8 및 AAV9를 포함할 수 있으나 이에 제한되지는 않는다.
한 실시양태에서, 제1 및 제2 벡터는 바이러스 DNA가 결여된, 본원에서 상호교환가능하게 사용되는 바이러스 벡터, 예를 들어 아데노-연관 바이러스 (AAV) 또는 재조합 AAV (rAAV)이다. 이중-벡터 시스템의 제1 벡터는 5'에서 3' 방향으로: 5'-역전된 말단 반복부 (5'-ITR) 서열; 하류 관심 폴리뉴클레오티드 (예를 들어, STRC)의 전사를 구동시킬 수 있는 프로모터 서열; 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열; 관심 단백질 (예를 들어, STRC)의 아미노 말단 (N-말단) 부분을 코딩하는 부분 코딩 서열인, 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 부분 코딩 서열; 인테인의 아미노 말단 단편 (N-인테인)을 코딩하는 서열인, 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 N-인테인을 코딩하는 서열; 폴리-아데닐화 (폴리A) 신호 서열; 및 3'-ITR 서열을 함유하는 뉴클레오티드 서열을 포함한다.
또 다른 실시양태에서, 제2 벡터는 5'에서 3' 방향으로: 5'-역전된 말단 반복부 (5'-ITR) 서열; 하류 관심 폴리뉴클레오티드 (예를 들어, STRC)의 전사를 구동시킬 수 있는 프로모터 서열; 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열; 인테인의 카르복시 말단 단편 (C-인테인)을 코딩하는 서열인, 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 C-인테인을 코딩하는 서열; 관심 단백질 (예를 들어, STRC)의 카르복시 말단 (C-말단) 부분을 코딩하는 부분 코딩 서열인, 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 부분 코딩 서열; 폴리-아데닐화 (폴리A) 신호 서열; 및 3'-ITR 서열을 포함한다.
추가 실시양태에서, 본 개시내용의 제1 벡터 및 제2 벡터가 바이러스 형질도입, 염화칼슘을 사용한 박테리아 형질전환, 박테리아 교배 또는 접합에 의한 박테리아 형질전환 또는 형질도입, 형질감염 (예를 들어, 전기천공, 인산칼슘, 리포솜-기반 형질감염), 유전자 총 등을 포함하나 이에 제한되지는 않는 임의의 수단에 의해 세포(들) (예를 들어, 숙주 세포, 포유동물 세포, 인간 세포, 박테리아 세포) 내로 삽입되는 경우에, 벡터는 각각 N-말단에서 C-말단 방향으로, 신호 펩티드 서열, 이에 연결된 관심 단백질 서열 (예를 들어, STRC)의 N-말단 부분, 이의 C-말단 단부에서 융합된 N-인테인 단백질 서열을 포함하는 제1 단백질 서열; 및 N-말단에서 C-말단 방향으로, 신호 펩티드 서열, 이에 연결된 C-인테인 단백질 서열, 이에 N-말단 단부에서 융합된 관심 단백질 서열 (예를 들어, STRC)의 C-말단 부분을 포함하는 제2 단백질 서열을 발현한다. 관심 단백질 (예를 들어, STRC)의 N-말단 부분 및 동일한 관심 단백질 (예를 들어, STRC)의 C-말단 부분의 인테인-매개 단백질 스플라이싱은 전장 관심 단백질 (예를 들어, STRC)의 발현을 일으킨다.
또 다른 실시양태는 이중-벡터 시스템의 신호 펩티드 서열을 제공하며, 여기서 신호 펩티드 서열은 이중-벡터 시스템에 의해 코딩되는 각각의 단백질 서열의 N-말단 단부에 위치할 수 있다. 관심 단백질 (예를 들어, STRC)의 N-말단 부분을 포함하는 제1 단백질 서열에서, 신호 펩티드 서열은 관심 단백질의 N-말단 부분의 코딩 영역뿐만 아니라 N-인테인의 상류일 수 있다. 관심 단백질 (예를 들어, STRC)의 C-말단 부분을 포함하는 제2 단백질 서열에서, 신호 펩티드 서열은 C-인테인뿐만 아니라 관심 단백질 (예를 들어, STRC)의 C-말단 부분의 코딩 영역의 상류일 수 있다.
본 개시내용의 또 다른 실시양태는 세포 내의 제1 벡터 및 제2 벡터가, 각각 동일한 신호 펩티드 서열을 함유하는, 각각 제1 단백질 서열 및 제2 단백질 서열을 발현하는 이중-벡터 시스템을 제공한다. 따라서, 동일한 신호 펩티드 서열은 제1 단백질 서열 및 제2 단백질 서열이 동일한 세포 구획으로 수송되도록 한다. 상이한 실시양태에서, 제1 및 제2 단백질 서열의 신호 펩티드 서열은 상이할 수 있지만, 이들 신호 펩티드 서열은 각각의 단백질 서열을 동일한 세포 구획으로 지시한다. 제1 및 제2 단백질 서열의 신호 펩티드 서열은 제1 단백질 서열 및 제2 단백질 서열을 동일한 세포 구획으로 수송하도록 구성될 수 있다. 그렇게 함에 있어서, 각각의 단백질 서열은 인테인-매개 단백질 융합이 발생하기에 충분히 근접할 수 있으며, 그에 의해 전장 관심 단백질 (예를 들어, STRC)을 형성한다. 신호 펩티드 서열은 관심 단백질 (예를 들어, STRC)과 회합될 수 있다. 추가 실시양태는 관심 단백질 이외의 다른 단백질과 회합된 신호 펩티드 서열을 코딩하는 신호 서열을 제공할 수 있으며, 여기서 제1 뉴클레오티드 서열의 신호 서열 및 제2 뉴클레오티드 서열의 신호 서열은 상이하고, 또한 신호 서열들이 상이한 신호 펩티드 서열들을 코딩하지만, 신호 서열들은 제1 단백질 서열 및 제2 단백질 서열을 동일한 세포 구획으로 수송하도록 구성된다. 본 개시내용의 또 다른 실시양태는 신호 서열이 인테인-매개 트랜스-스플라이싱을 파괴하지 않으면서 2개의 단편을 동일한 세포 또는 세포내 구획으로 지시하도록 하는 신호 서열 또는 신호 서열들을 제공한다. 신호 서열은 제1 단백질 서열 및 제2 단백질 서열이 서로에 대해 충분히 근접하여 관심 단백질 (예를 들어, STRC)의 N-말단 부분 및 관심 단백질 (예를 들어, STRC)의 C-말단 부분이 펩티드 결합을 통해 전장 관심 단백질 (예를 들어, STRC)을 형성하게 하는 것을 보장하는 데 특히 유용할 수 있다.
본 개시내용의 한 실시양태에서, 신호 서열은 관심 단백질 (예를 들어, STRC)의 신호 펩티드 서열을 코딩하는 신호 서열에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함할 수 있다. 예를 들어, 신호 서열은 STRC 단백질 신호 펩티드를 코딩하는 유전자 서열의 서열식별번호: 11에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함할 수 있거나, 또는 신호 서열은, 예를 들어 관심 단백질 및 관심 단백질의 각각의 부분을 동일한 세포 구획으로 지시하는 임의의 신호 서열 (예를 들어, 서열식별번호: 9 또는 서열식별번호: 11)로 이루어진 핵산 서열을 포함할 수 있다. 또 다른 실시양태는 관심 단백질 (예를 들어, STRC; 서열식별번호: 10; 서열식별번호: 12)의 신호 펩티드 서열에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 갖는 신호 펩티드 서열을 코딩하는 신호 서열을 제공할 수 있다. 예를 들어, 신호 펩티드 서열은 STRC 단백질 신호 펩티드의 서열식별번호: 10 또는 서열식별번호: 12에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 포함할 수 있거나, 또는 신호 펩티드 서열은 서열식별번호: 10 또는 서열식별번호: 12로 이루어진 아미노산 서열을 포함할 수 있다.
추가 실시양태는 관심 단백질 (예를 들어, STRC)의 N-말단 부분을 코딩하는 부분 코딩 서열을 제공할 수 있으며, 여기서 부분 코딩 서열은 관심 단백질의 N-말단 부분을 코딩하는 코딩 서열 (예를 들어, STRC; 서열식별번호: 6, 8, 15, 16, 25 또는 26)에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함한다. 예를 들어, STRC 단백질의 N-말단 부분을 코딩하는 부분 코딩 서열 (상이한 신호 서열과 교환가능할 수 있는 신호 서열을 포함함)은 하기 서열에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함할 수 있다.
STRC 단백질의 인간 N-말단 부분을 코딩하는 부분 코딩 서열 (개시 코돈 ATG (볼드체) 및 신호 서열 (소문자, 이탤릭체 및 밑줄표시) 포함)은 하기와 같을 수 있다:
STRC 단백질의 뮤린 N-말단 부분을 코딩하는 부분 코딩 서열 (개시 코돈 ATG (볼드체) 및 신호 서열 (소문자, 이탤릭체 및 밑줄표시) 포함)은 하기와 같을 수 있거나:
또는 STRC 단백질의 N-말단 부분을 코딩하는 부분 코딩 서열은 서열식별번호: 55 또는 56으로 이루어진 핵산 서열을 포함할 수 있다. 또 다른 실시양태는 관심 단백질 (예를 들어, STRC; 서열식별번호: 25 또는 26)에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 갖는 관심 단백질 (예를 들어, STRC)의 N-말단 부분 (개시 코돈 ATG에 상응하는 메티오닌 및 신호 펩티드 서열을 포함함)을 제공할 수 있다. 예를 들어, STRC 단백질의 N-말단 부분 (개시 코돈 ATG에 상응하는 메티오닌 및 STRC 신호 펩티드 서열 포함, 이는 교환가능할 수 있음)은 서열식별번호: 15 또는 16의 서열에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 포함할 수 있거나, 또는 STRC 단백질의 N-말단 부분은 서열식별번호: 15 또는 16으로 이루어진 아미노산 서열을 포함할 수 있다. 제1 벡터의 제1 뉴클레오티드 서열은 자신의 신호 서열 (예를 들어, 서열식별번호: 10 또는 12) 또는 대안적으로 상이한 신호 서열을 포함하는 관심 단백질의 N-말단 부분 (예를 들어, STRC; 서열식별번호: 15 또는 16)을 코딩하는 부분 코딩 서열 및 스플라이스 공여자 서열 (예를 들어, N-말단 인테인 (N-인테인); 서열식별번호: 14)을 코딩하는 서열을 포함할 수 있다.
한 실시양태에서, 관심 단백질 (예를 들어, STRC)의 C-말단 부분을 코딩하는 부분 코딩 서열 (개시 코돈 ATG에 상응하는 메티오닌 및 신호 서열 포함, 이는 교환가능할 수 있음; 임의로 링커 서열 및 Myc 태그 서열 포함)이며, 여기서 부분 코딩 서열은 관심 단백질 (예를 들어, STRC; 서열식별번호: 18, 20, 23, 24, 25 또는 26)에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함한다. 예를 들어, STRC 단백질의 C-말단 부분을 코딩하는 부분 코딩 서열은 하기 서열에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함할 수 있다.
STRC 단백질의 인간 C-말단 부분을 코딩하는 부분 코딩 서열은 하기와 같을 수 있다 (즉, ATG 개시 코돈, 신호 서열 또는 스플라이스 수용자 서열이 없음):
STRC 단백질의 뮤린 C-말단 부분을 코딩하는 부분 코딩 서열은 하기와 같을 수 있거나:
또는 STRC 단백질의 C-말단 부분을 코딩하는 부분 코딩 서열은 서열식별번호: 57 또는 58로 이루어진 핵산 서열을 포함할 수 있다. 또 다른 실시양태는 관심 단백질 (예를 들어, STRC; 서열식별번호: 25 또는 26)에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 갖는 관심 단백질 (예를 들어, STRC)의 C-말단 부분 (개시 코돈 ATG에 상응하는 메티오닌, 신호 펩티드 서열; 임의로 링커 서열 및 Myc 태그 서열 포함)을 제공할 수 있다. 예를 들어, STRC 단백질의 C-말단 부분 (개시 코돈 ATG에 상응하는 메티오닌, STRC 신호 펩티드 서열; 임의로 링커 서열 및 Myc 태그 서열 포함)은 서열식별번호: 23 또는 24의 서열에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 포함할 수 있거나, 또는 STRC 단백질의 C-말단 부분은 서열식별번호: 23 또는 24로 이루어진 아미노산 서열을 포함할 수 있다. 제2 벡터의 제2 뉴클레오티드 서열은 자신의 신호 서열 (예를 들어, 서열식별번호: 10 또는 12) 또는 대안적으로 상이한 신호 서열을 포함하는 관심 단백질의 C-말단 부분 (예를 들어, STRC; 서열식별번호: 23 또는 24)을 코딩하는 부분 코딩 서열 및 스플라이스 수용자 서열 (예를 들어, C-말단 인테인 (C-인테인); 서열식별번호: 22)을 코딩하는 서열을 포함할 수 있다.
한 실시양태는 서열식별번호: 42에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함하는 N-인테인 서열 또는 서열식별번호: 45에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 코딩하는 N-인테인 서열을 제공할 수 있다. 다른 실시양태는 서열식별번호: 42의 핵산 서열로 이루어진 N-인테인 서열 또는 서열식별번호: 45로 이루어진 아미노산 서열을 코딩하는 N-인테인 서열에 관한 것일 수 있다.
또 다른 실시양태는 서열식별번호: 46에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함하는 C-인테인 서열 또는 서열식별번호: 49에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 코딩하는 C-인테인 서열을 제공한다. 다른 실시양태는 서열식별번호: 46의 핵산 서열로 이루어진 C-인테인 서열 또는 서열식별번호: 49로 이루어진 아미노산 서열을 코딩하는 C-인테인 서열에 관한 것일 수 있다.
추가 실시양태에서, 본 개시내용의 이중-벡터 시스템은 관심 단백질의 N-말단 부분 (예를 들어, STRC; 서열식별번호: 15 또는 16)을 코딩하는 제1 뉴클레오티드 서열을 제공하며, 여기서 제1 뉴클레오티드 서열은 관심 단백질 (예를 들어, STRC)의 N-말단 부분의 부분 코딩 서열 (5')의 일부를 형성하거나 또는 그와 별개일 수 있는 관심 단백질의 신호 서열, 및 관심 단백질 (예를 들어, STRC)의 N-말단 부분의 부분 코딩 서열의 일부를 형성하거나 또는 그와 별개일 수 있는 스플라이스 공여자 서열 (예를 들어, N-인테인 서열)을 포함하나 이에 제한되지는 않고, 여기서 제1 뉴클레오티드 서열은 관심 단백질 (예를 들어, STRC)의 N-말단 부분을 코딩하는 뉴클레오티드 서열에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함할 수 있고, 관심 단백질의 내인성 신호 서열 또는 외인성 신호 서열, 관심 단백질의 N-말단 부분의 부분 코딩 서열 (5') 및 스플라이스 공여자 서열 (예를 들어, N-인테인 서열)을 포함하나 이에 제한되지는 않는다 (서열식별번호: 5 또는 7). 한 실시양태는, 예를 들어 서열식별번호: 5 또는 7에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함하는 제1 뉴클레오티드 서열을 제공할 수 있거나, 또는 제1 뉴클레오티드 서열은 서열식별번호: 5 또는 7로 이루어진 핵산 서열을 포함할 수 있다.
또 다른 실시양태는 관심 단백질 (예를 들어, STRC)의 N-말단 부분을 포함하는 서열에 대해 적어도 80% (예를 들어, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 코딩하는 제1 뉴클레오티드 서열을 제공하며, 여기서 제1 뉴클레오티드 서열은 관심 단백질 (예를 들어, STRC)의 N-말단 부분의 부분 코딩 서열 (5')의 일부를 형성하거나 또는 그와 별개일 수 있는 관심 단백질의 내인성 신호 서열 또는 외인성 신호 서열, 및 관심 단백질 (예를 들어, STRC)의 N-말단 부분의 부분 코딩 서열의 일부를 형성하거나 또는 그와 별개일 수 있는 스플라이스 공여자 서열 (예를 들어, N-인테인 서열)을 포함하나 이에 제한되지는 않는다. 추가 실시양태는, 예를 들어 서열식별번호: 6 또는 8에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 코딩하는 제1 뉴클레오티드 서열을 제공할 수 있거나, 또는 제1 뉴클레오티드 서열은 서열식별번호: 6 또는 8로 이루어진 아미노산 서열을 코딩할 수 있다.
본 개시내용의 이중-벡터 시스템의 추가 실시양태는 관심 단백질의 C-말단 부분 (예를 들어, STRC; 서열식별번호: 23 또는 24)을 코딩하는 제2 뉴클레오티드 서열을 제공하며, 여기서 제2 뉴클레오티드 서열은 관심 단백질 (예를 들어, STRC)의 C-말단 부분의 부분 코딩 서열 (3')의 일부를 형성하거나 또는 그와 별개일 수 있는 관심 단백질의 내인성 신호 서열 또는 외인성 신호 서열, 및 관심 단백질 (예를 들어, STRC)의 C-말단 부분의 부분 코딩 서열의 일부를 형성하거나 또는 그와 별개일 수 있는 스플라이스 수용자 서열 (예를 들어, C-인테인 서열)을 포함하나 이에 제한되지는 않고, (여기서 제2 뉴클레오티드 서열은 일부 실시양태에서 링커 서열 및 Myc-태그 서열을 임의로 포함할 수 있음), 여기서 제2 뉴클레오티드 서열은 관심 단백질 (예를 들어, STRC)의 C-말단 부분을 코딩하는 뉴클레오티드 서열에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함할 수 있고, 관심 단백질의 내인성 신호 서열 또는 외인성 신호 서열, 관심 단백질의 C-말단 부분의 부분 코딩 서열 (3') 및 스플라이스 수용자 서열 (예를 들어, C-인테인 서열 (및 임의로 링커 서열 및 Myc-태그 서열을 포함함))을 포함하나 이에 제한되지는 않는다 (서열식별번호: 17 또는 19). 한 실시양태는, 예를 들어 서열식별번호: 17 또는 19에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 핵산 서열을 포함하는 제2 뉴클레오티드 서열을 제공할 수 있거나, 또는 제2 뉴클레오티드 서열은 서열식별번호: 17 또는 19로 이루어진 핵산 서열을 포함할 수 있다.
또 다른 실시양태는 관심 단백질의 신호 서열, C-인테인 서열 및 관심 단백질의 C-말단 부분의 부분 코딩 서열 (3') (및 임의로 링커 서열 및 Myc-태그 서열을 포함함)을 포함하나 이에 제한되지는 않는 관심 단백질 (예를 들어, STRC)의 C-말단 부분을 포함하는 서열에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 코딩하는 제2 뉴클레오티드 서열을 제공한다. 추가 실시양태는 서열식별번호: 18 또는 20에 대해 적어도 5% (예를 들어, 6%, 7%, 8%, 9%, 10%, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 85%, 90%, 95%, 97%, 99%, 100%) 동일성의 아미노산 서열을 코딩하는 제2 뉴클레오티드 서열을 제공할 수 있거나, 또는 제2 뉴클레오티드 서열은 서열식별번호: 18 또는 20으로 이루어진 아미노산 서열을 코딩할 수 있다.
추가 실시양태에서, 본 개시내용의 이중-벡터 시스템은 5'에서 3' 방향으로, ITR, 프로모터 (예를 들어, CMV 프로모터), 관심 부분 코딩 서열 (예를 들어, 5' Strc), 스플라이스 공여자 서열 (예를 들어, 5' 인테인) 및 ITR을 갖는 제1 뉴클레오티드 서열 (예를 들어, AAV 벡터 1); 및 ITR, 프로모터 (예를 들어, CMV 프로모터), 스플라이스 수용자 서열 (예를 들어, 3' 인테인), 관심 부분 코딩 서열 (예를 들어, 3' Strc) 및 ITR을 갖는 제2 뉴클레오티드 서열 (예를 들어, AAV 벡터 2)을 제공한다 (도 31a). 번역을 겪으면, 제1 및 제2 뉴클레오티드 서열은 다수의 변이체를 생성할 수 있으며, 이들은 서열식별번호: 26의 위치 747 및 970에서의 천연 시스테인, 즉 Cys747 및 Cys970 (또는 서열식별번호: 25의 위치 709 및 934에서의 천연 시스테인, 즉 Cys709 및 Cys934)을 이용하여 스플라이싱되는 경우에, 전장 STRC 단백질 및 n-인테인 및 c-인테인을 포함하는 절제된 인테인을 형성한다. 도 31a는 4개의 상이한 이중 벡터 변이체를 포함하는 8개의 AAV2 플라스미드를 예시한다.
예를 들어, 변이체 1은 N-말단에서 C-말단 방향으로, 신호 펩티드 서열, 관심 단백질의 N-말단 부분 (예를 들어, ~80 kD의 n-STRC), 스플라이스 부위 (예를 들어, Ser746) 및 스플라이스 공여자 서열 (n-인테인)을 포함하는 제1 단백질 서열; 및 N-말단에서 C-말단 방향으로, 스플라이스 수용자 서열 (c-인테인), 스플라이스 부위 (예를 들어, Cys747) 및 관심 단백질의 C-말단 부분 (예를 들어, ~117 kD의 c-STRC)을 포함하는 제2 단백질 서열을 포함한다. 변이체 2는, 예를 들어 N-말단에서 C-말단 방향으로, 신호 펩티드 서열, 관심 단백질의 N-말단 부분 (예를 들어, ~105 kD의 n-STRC), 스플라이스 부위 (예를 들어, Ala969) 및 스플라이스 공여자 서열 (n-인테인)을 포함하는 제1 단백질 서열; 및 N-말단에서 C-말단 방향으로, 스플라이스 수용자 서열 (c-인테인), 스플라이스 부위 (예를 들어, Cys970) 및 관심 단백질의 C-말단 부분 (예를 들어, ~92 kD의 c-STRC)을 포함하는 제2 단백질 서열을 포함한다. 예를 들어, 변이체 3은 N-말단에서 C-말단 방향으로, 신호 펩티드 서열, 관심 단백질의 N-말단 부분 (예를 들어, ~80 kD의 n-STRC), 스플라이스 부위 (예를 들어, Ser746) 및 스플라이스 공여자 서열 (n-인테인)을 포함하는 제1 단백질 서열; 및 N-말단에서 C-말단 방향으로, 신호 펩티드 서열, 스플라이스 수용자 서열 (c-인테인), 스플라이스 부위 (예를 들어, Cys747) 및 관심 단백질의 C-말단 부분 (예를 들어, ~117 kD의 c-STRC)을 포함하는 제2 단백질 서열을 포함한다. 변이체 4는, 예를 들어 N-말단에서 C-말단 방향으로, 신호 펩티드 서열, 관심 단백질의 N-말단 부분 (예를 들어, ~105 kD의 n-STRC), 스플라이스 부위 (예를 들어, Ala969) 및 스플라이스 공여자 서열 (n-인테인)을 포함하는 제1 단백질 서열; 및 N-말단에서 C-말단 방향으로, 신호 펩티드 서열, 스플라이스 수용자 서열 (c-인테인), 스플라이스 부위 (예를 들어, Cys970) 및 관심 단백질의 C-말단 부분 (예를 들어, ~92 kD의 c-STRC)을 포함하는 제2 단백질 서열을 포함한다.
번역된 변이체 서열의 단백질 스플라이싱 시, 전장 관심 단백질 (예를 들어, STRC)이 형성된다. 예를 들어, N-말단에서 C-말단 방향으로, 관심 단백질 (n-STRC)의 N-말단 부분은 관심 단백질 (예를 들어, c-STRC)의 C-말단 부분에 연결될 수 있다. N-말단 및 C-말단 단부의 스플라이싱은 스플라이스 공여자 서열 및 스플라이스 수용자 서열의 절제를 유발한다. 예를 들어, 절제된 스플라이스 서열은 전장 스플라이스 서열 (예를 들어, n-인테인 및 c-인테인의 절제된 인테인)을 형성할 수 있다 (도 31a).
도 31c는 변이체 3의 N-말단 부분 및 C-말단 부분 (c+n) 둘 다로 형질감염된 HEK 세포가, 단지 C-말단 부분 (c)만을 갖는 변이체 3 또는 C-말단 부분 단독 (c) 또는 이와 함께 N-말단 부분 (c+n)을 갖는 변이체 1과는 대조적으로, 전장 STRC의 발현을 일으켰다는 것을 입증한다. 변이체 1과 변이체 3 사이의 유일한 차이는 C-말단 부분에 신호 서열이 존재한다는 것이다. 따라서, 도 31c는 N-말단 부분 및 C-말단 부분 둘 다에서의 신호 서열이 각각의 부분을 세포의 동일한 세포 구획으로 지시하여, 단백질 스플라이싱이 전장 STRC를 형성할 수 있게 한다는 것을 입증한다.
추가 실시양태는 제1 벡터 및 제2 벡터를 포함하는, 본원에 기재된 이중-벡터 시스템을 함유하는 세포 (예를 들어, 숙주 세포, 포유동물 세포, 인간 세포, 박테리아 세포)를 제공한다. 한 실시양태에서, 세포는 내이 세포, 내유모 세포 또는 외유모 세포일 수 있다. 일부 실시양태는 포유동물 세포 (예를 들어, 인간, 개, 고양이, 말, 뮤린)인 세포에 관한 것일 수 있다. 다른 실시양태는 귀 세포 (예를 들어, 내이 세포, 외이 세포, 내유모 세포, 외유모 세포)를 제공할 수 있다. 본 개시내용의 세포는 생체내 또는 시험관내일 수 있다. 일부 실시양태에서, 세포는 관련 기술분야에 일반적으로 공지된 임의의 다수의 공지된 형질감염 및 형질전환 기술을 사용하여 본 개시내용의 이중-벡터 시스템의 제1 벡터 및 제2 벡터로 형질감염 또는 형질전환될 수 있다. 예를 들어, 문헌 [Graham et al. (1973) Virology, 52:456, Sambrook et al. (1989) Molecular Cloning, a laboratory manual, Cold Spring Harbor Laboratories, New York, Davis et al. (1986) Basic Methods in Molecular Biology, Elsevier, and Chu et al. (1981) Gene 13:197]을 참조하며, 이들 모두는 그 전문이 본원에 참조로 포함된다. 본 개시내용의 이중-벡터 시스템의 제1 벡터 및 제2 벡터는 바이러스 형질도입, 염화칼슘을 사용한 박테리아 형질전환, 박테리아 교배 또는 접합에 의한 박테리아 형질전환 또는 형질도입, 형질감염 (예를 들어, 전기천공, 인산칼슘, 리포솜-기반 형질감염), 유전자 총 등을 포함하나 이에 제한되지는 않는 임의의 수단에 의해 본원에 기재된 세포(들) 내로 삽입될 수 있다.
또 다른 실시양태는 본원에 기재된 이중-벡터 시스템 및 제약상- 또는 생리학상-허용되는 비히클 (예를 들어, 희석제, 담체, 부형제)을 포함하는 조성물 또는 제약 조성물에 관한 것일 수 있다. 돌연변이와 연관된 질환 또는 상태의 치료를 위해 본원에서 고려되는 조성물은 본원에 기재된 이중-벡터 시스템을 포함할 수 있다. 치료 목적을 위해, 본원에 개시된 방법에 따라 적절하게 프로세싱되는 경우에, 본원에 기재된 바와 같은 질환 또는 상태 (예를 들어, 상염색체 열성 DFNB16 청력 상실)를 유발하거나 또는 이에 기여하는 돌연변이를 포함하는 게놈에서 전장 관심 단백질 (예를 들어, STRC 단백질)의 발현을 일으키는 관심 폴리뉴클레오티드 (예를 들어, STRC) 또는 그의 단편을 포함하는 조성물이 질환 또는 상태에 의해 영향을 받는 신체의 영역 (예를 들어, 와우, 내이)에 직접 투여될 수 있다. 일부 실시양태에서, 조성물은 제약상 허용되는 완충제, 예컨대 생리 염수 중에 제제화된다. 비제한적 투여 방법은 귀, 내이, 와우관 또는 와우관 주위의 외림프-충전된 공간 (예를 들어, 고실계 및 전정계) 내로 주사하는 것을 포함한다. 고칼륨 내림프액으로 충전된 와우관 내로의 주사는 유모 세포에 대한 직접적 접근을 제공할 수 있다. 그러나, 이러한 섬세한 유체 환경에 대한 변경은 와우내 잠재력을 파괴하여, 주사-관련 독성에 대한 위험을 높일 수 있다. 와우관을 둘러싸는 외림프-충전된 공간, 고실계 및 전정계는 난원창 또는 원형창 막을 통해 중이로부터 접근될 수 있다. 내이 내로의 유일한 비-골성 개구부인 원형창 막은 많은 동물 모델에서 비교적 용이하게 접근가능하고, 이 경로를 사용한 바이러스 벡터의 투여는 잘 허용된다. 인간에서, 와우 이식물 배치는 상용적으로 원형창 막을 통한 외과적 전극 삽입에 의존한다.
사용 방법
한 실시양태는 치료를 필요로 하는 대상체에게 유효량의 본원에 기재된 이중-벡터 시스템을 투여하는 것을 포함하는, 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템; 캡시드, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈, 렌티바이러스)을 사용하는 방법을 제공할 수 있으며, 여기서 방법은 결함성 또는 돌연변이된 유전자로부터 유발된 질환, 상태 또는 그의 증상을 치료 및/또는 감소 및/또는 예방할 수 있다.
또 다른 실시양태는 (예를 들어, 대상체의) 세포를, 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템) 및 제약상- 또는 생리학상-허용되는 비히클 (예를 들어, 담체, 희석제, 부형제)을 포함하는 조성물과 접촉시키는 것을 포함하는 방법에 관한 것일 수 있다. 세포 (예를 들어, 대상체의 세포)와의 접촉 단계는, 예를 들어 서열식별번호: 33 (도 2a-2c) 또는 서열식별번호: 38 (도 4a-4d)을 포함하는 벡터 (예를 들어, 플라스미드, 트랜스스플라이싱 플라스미드, 바이러스 벡터, 아데노바이러스, AAV, AAV 게놈)의 뉴클레오티드 서열의 전달을 일으킬 수 있으며, 여기서 세포는 전장 관심 단백질 (예를 들어, STRC; 인간 서열식별번호: 2 또는 25; 뮤린 서열식별번호: 4 또는 26)을 발현할 수 있다. 대상체의 세포와의 접촉 단계는 (각각 제1 벡터 및 제2 벡터의) 제1 뉴클레오티드 서열 및 제2 뉴클레오티드 서열의 전달을 일으킬 수 있으며, 여기서 세포는 관심 단백질 (예를 들어, STRC)의 N-말단 부분 및 관심 단백질의 C-말단 부분을 발현할 수 있고, 관심 단백질 (예를 들어, STRC)의 N-말단 부분 및 관심 단백질의 C-말단 부분은 펩티드 결합에 의해 연결되어 전장 관심 단백질 (예를 들어, STRC; 인간 서열식별번호: 2 또는 25; 뮤린 서열식별번호: 4 또는 26)을 형성한다.
한 실시양태는 상염색체 열성 청력 상실의 치료를 필요로 하는 대상체에게 유효량의 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템), 또는 본원에 기재된 조성물, 또는 본 개시내용의 벡터 시스템 (예를 들어, 이중-벡터 시스템) 또는 본 개시내용의 조성물을 함유하는 세포, 또는 관심 단백질 (예를 들어, STRC; 서열식별번호: 25; 서열식별번호: 26)을 코딩하는 적어도 1개의 뉴클레오티드 서열 (예를 들어, STRC; 서열식별번호: 5 서열식별번호: 7; 서열식별번호: 17; 서열식별번호: 19; 서열식별번호: 30; 서열식별번호: 32) 또는 관심 단백질 (예를 들어, STRC; 서열식별번호: 25; 서열식별번호: 26) 자체 또는 관심 단백질의 부분 (예를 들어, 서열식별번호: 6 - 서열식별번호: 16; 서열식별번호: 18 - 서열식별번호: 24)을 포함하는 벡터 또는 조성물을 투여하는 것을 포함하는, 대상체에서 상염색체 열성 청력 상실을 치료하는 방법을 제공할 수 있으며, 여기서 투여는 상염색체 열성 청력 상실 또는 그의 증상의 감소 또는 회복을 가져올 수 있다. 일부 실시양태에서, 치료를 필요로 하는 대상체는 치료 후 대상체가 69 dB 이하 (예를 들어, 60 dB, 55 dB, 50 dB, 45 dB, 40 dB, 35 dB, 30 dB, 26 dB, 25 dB, 20 dB, 15 dB, 10 dB, 5 dB, 0 dB)의 청력 수준을 갖는 경우에 성공적으로 치료되었을 것이다. 일반적으로, 극심한 청력 상실을 갖는 대상체는 95 dB 미만의 소리를 들을 수 없고; 중증 청력 상실을 갖는 대상체는 70 dB 내지 94 dB 미만의 소리를 들을 수 없고; 중등도 청력 상실 대상체는 40 dB 내지 69 dB 미만의 소리를 들을 수 없고; 경도 청력 상실을 갖는 대상체는 26 dB 내지 40 dB 미만의 소리를 들을 수 없다. 그러나, 예를 들어 상염색체 열성 청력 상실을 포함한 청력 상실을 앓고 있는 대상체는 본원에 기재된 임의의 방법에 의해 치료될 수 있으며, 따라서 청력 상실 또는 그의 증상의 감소 및/또는 청력 (또는 대상체에서의 청각 기능)의 회복 또는 개선 및/또는 청력의 유지를 유발할 수 있다. 정상 청력을 갖는 대상체는 25 dB 이하 (예를 들어, 20 dB, 15 dB, 10 dB, 5 dB, 0 dB)의 청력 소리를 특징으로 할 수 있다. 일부 실시양태에서, 상염색체 열성 청력 상실은 DFNB16이다.
추가 실시양태는 청력 상실을 특징으로 하는 병리상태 또는 질환의 치료 및/또는 예방을 필요로 하는 대상체에게 유효량의 본원에 기재된 이중-벡터 시스템, 본 개시내용에 따른 세포 또는 본원에 기재된 조성물 또는 제약 조성물을 투여하는 것을 포함하는, 청력 상실을 특징으로 하는 병리상태 또는 질환을 치료 및/또는 예방하는 방법을 제공할 수 있다. 본 개시내용의 세포는 내이 세포, 내유모 세포, 외유모 세포, 생체내 세포, 시험관내 세포 등 또는 상기 중 임의의 것의 조합일 수 있다.
폴리뉴클레오티드 전달
이들 접근법에서의 치료 성공은 와우 내 코르티 기관에서의 관련 치료 세포 표적으로의 외인성 유전자 구축물의 안전하고 효율적인 전달에 유의하게 의존한다. 코르티 기관은 2가지 부류의 감각 유모 세포를 포함한다: 소리에 의해 운반되는 기계적 정보를 뉴런 구조로 전송되는 전기적 신호로 전환시키는 내유모 세포 및 복잡한 청각 기능에 요구되는 과정인 와우 반응을 증폭시키고 조정하는 역할을 하는 외유모 세포.
핵산을 세포로 전달하는 방법은 일반적으로 관련 기술분야에 공지되어 있고, 트랜스진을 함유하는 바이러스 (이는 또한 바이러스 입자로도 지칭될 수 있음)를 생체내 내이 세포로 전달하는 방법은 본원에 기재되어 있다. 본원에 기재된 바와 같이, 약 108 내지 약 1012개 바이러스 입자가 대상체에게 투여될 수 있고, 바이러스는 적합한 부피 (예를 들어, 10 μL, 50 μL, 100 μL, 500 μL 또는 1000 μL)의, 예를 들어 인공 외림프 용액 중에 현탁될 수 있다.
본원에 기재된 바와 같은 역전된 말단 반복부 (ITR), 프로모터 (예를 들어, 에스핀 프로모터, PCDH15 프로모터, PTPRQ 프로모터, Myo6 프로모터, KCNQ4 프로모터, Myo7a 프로모터, 시냅신 프로모터, GFAP 프로모터, CMV 프로모터, CAG 프로모터, CBH 프로모터, CBA 프로모터, U6 프로모터 및 TMHS (LHFPL5) 프로모터), 신호 서열, 관심 단백질 (예를 들어, STRC 단백질)을 코딩하는 폴리뉴클레오티드 및 폴리아데닐화 (폴리A) 서열, 및 일부 실시양태에서, c-myc 태그를 연결하기 위한 링커 서열을 함유하는 바이러스는 임의의 수의 수단을 사용하여 내이 세포 (예를 들어, 와우 내의 세포)에 전달될 수 있다. 예를 들어, 본원에 기재된 바와 같은 이중-벡터 인테인-매개 단백질 트랜스-스플라이싱 시스템을 함유하는 바이러스 입자를 포함하는 조성물의 치료 유효량은 전형적으로 비교적 간단한 (예를 들어, 외래환자) 절차로 원형창 또는 난원창 또는 난형낭을 통해 주사될 수 있다. 일부 실시양태에서, 본원에 기재된 바와 같은 이중-벡터 인테인-매개 단백질 트랜스-스플라이싱 시스템 (예를 들어, 이중-AAV 인테인-매개 STRC 단백질 시스템)을 함유하거나 또는 상이한 바이러스 입자의 1개 이상의 세트를 함유하는 바이러스 입자의 치료 유효량을 포함하는 조성물은 수술 (예를 들어, 와우개창술 또는 반고리관절개술) 동안 귀 안의 적절한 위치로 전달될 수 있다.
추가로, 고막을 가로지른 및/또는 원형창 또는 난형낭을 통한 작용제의 전달을 용이하게 하는 전달 비히클 (예를 들어, 중합체)이 이용가능하고, 임의의 이러한 전달 비히클은 본원에 기재된 바이러스를 전달하는 데 사용될 수 있다. 예를 들어, 전달 비히클에 대해 문헌 [Arnold et al., 2005, Audiol. Neurootol., 10:53-63] (그 전문이 본원에 참조로 포함됨)을 참조한다.
본원에 기재된 조성물 및 방법은 내이 세포, 예를 들어 와우 세포로의 핵산의 고도로 효율적인 전달을 가능하게 한다. 예를 들어, 관심 단백질 (예를 들어, STRC 단백질) 또는 그의 단편을 코딩하는 폴리뉴클레오티드는 바이러스 벡터 내로 클로닝될 수 있고, 발현은 그의 내인성 프로모터로부터, 바이러스 역전된 말단 반복부로부터 또는 관심 표적 세포 유형에 특이적인 프로모터로부터 구동될 수 있다. 사용될 수 있는 다른 바이러스 벡터는, 예를 들어 백시니아 바이러스, 소 유두종 바이러스 또는 포진 바이러스, 예컨대 엡스타인-바르 바이러스를 포함한다. 바이러스 벡터는 임상 환경에서 사용되었다. 일부 실시양태에서, 바이러스 벡터 (예를 들어, rAAV)는 큰 (예를 들어, Strc 유전자) 폴리뉴클레오티드를 단편들로 투여하는 데 사용될 수 있다. 일부 실시양태에서, 바이러스 벡터는 신체의 특정한 영역에 Strc 폴리뉴클레오티드 단편을 투여하는 데 사용될 수 있다.
예를 들어, 본원에 기재된 조성물 및 방법은 내유모 및/또는 외유모 세포의 적어도 65% 이상 (예를 들어, 70%, 75%, 80%, 85%, 90%, 91%, 92%, 93%, 94%, 95%, 96%, 97%, 98%, 99%)으로의 관심 폴리뉴클레오티드 (예를 들어, Strc)의 전달 및 그에서의 발현, 또는 외유모 세포의 적어도 65% 이상 (예를 들어, 70%, 75%, 80%, 85%, 90%, 91%, 92%, 93%, 94%, 95%, 96%, 97%, 98%, 99%)으로의 전달 및 그에서의 발현을 가능하게 한다.
본원에 기재된 이중-벡터 인테인-매개 시스템을 사용하여 전달된 STRC 폴리뉴클레오티드의 발현은 내유모 및 외유모 세포의 개선된 구조 및 기능을 가져와, 청력이 연장된 기간 (예를 들어, 수일, 수주, 수개월, 수년, 수십년, 평생) 동안 회복되도록 할 수 있다. 한 실시양태에서, 청력 상실은 STRC 유전자 내의 돌연변이에 의해 유발된 상염색체 열성 유형의 비-증후군성 난청인 DFNB16을 앓고 있는 대상체에서 회복될 수 있다. STRC 및 스테레오실린 (STRC) 단백질의 정상 발현은 청각 기능에 필수적이다.
본원에 기재된 바와 같이, 아데노-연관 바이러스 (AAV)는 핵산 (예를 들어, STRC 폴리펩티드를 코딩하는 폴리뉴클레오티드)을 내이 세포로 전달하는 데 특히 효율적이다. Anc80 벡터는 60% 이상 (예를 들어, 70%, 80%, 90%, 95%, 100%)의 내유모 또는 외유모 세포를 유리하게 형질도입시킨 내이 유모 세포 표적화 AAV의 예이다. 한 실시양태는 Anc80 조상 캡시드 단백질의 부류 내에 속하는 조상 캡시드 단백질, 예를 들어 국제 공개 번호 WO 2018/145111 (PCT/US2018/017104)에 기재된 Anc80-0065 (이는 Anc80에 관하여 그 전문이 본원에 참조로 포함됨)를 이용할 수 있다. WO 2015/054653 (이는 또한 그 전문이 본원에 참조로 포함됨)에는 Anc80 조상 캡시드 단백질의 부류 내에 속하는 다수의 추가의 조상 캡시드 단백질이 기재되어 있다.
특정한 실시양태에서, 아데노-연관 바이러스 (AAV)는 유모 세포에 대한 천연 또는 조작된 향성을 갖는 조상 AAV 캡시드 단백질을 함유한다. 일부 실시양태에서, 바이러스는 관심 폴리펩티드 (예를 들어, STRC 단백질)를 코딩하는 관심 폴리뉴클레오티드를 대상체 (예를 들어, DFNB16 및/또는 STRC 유전자 내의 돌연변이를 앓고 있는 대상체)의 내이로 전달하는 내이 유모 세포 표적화 AAV이다. 일부 실시양태에서, 바이러스는 정제된 캡시드 폴리펩티드를 포함하는 AAV이다. 일부 실시양태에서, 바이러스는 인공이다. 일부 실시양태에서, 바이러스는 AAV2보다 더 낮은 혈청유병률을 갖는 AAV이다. 일부 실시양태에서, 바이러스는 엑솜-연관 AAV이다. 일부 실시양태에서, 바이러스는 엑솜-연관 AAV1이다. 일부 실시양태에서, 바이러스는 Anc80 캡시드 단백질에 대해 적어도 95% 아미노산 서열 동일성 또는 상동성을 갖는 캡시드 단백질을 포함한다.
관심 폴리뉴클레오티드 (예를 들어, STRC)의 발현은 이종 프로모터 (예를 들어, CMV 프로모터, Espin 프로모터, PCDH15 프로모터, PTPRQ 프로모터, TMHS (LHFPL5) 프로모터)에 의해 지시될 수 있다. 본원에 사용된 "이종 프로모터"는 그 서열의 발현을 자연적으로 지시하지 않는 (즉, 자연에서 그 서열과 함께 발견되지 않는) 프로모터를 지칭한다.
트랜스진을, 예를 들어 Anc80 캡시드 단백질을 함유하는 바이러스 내로 패키징하는 방법은 관련 기술분야에 공지되어 있고, 통상적인 분자 생물학 및 재조합 핵산 기술을 이용한다. 한 실시양태에서, Anc80 캡시드 단백질을 코딩하는 핵산 서열을 포함하는 구축물, 및 Anc80 캡시드 단백질 내에 패키징되도록 하는 적합한 역전된 말단 반복부 (ITR)가 플랭킹된 STRC 단백질의 N-말단 및 C-말단 부분을 코딩하는 폴리뉴클레오티드의 단편을 보유하는 구축물이 제공된다.
관심 폴리뉴클레오티드 (예를 들어, STRC)는, 예를 들어 패키징 숙주 세포를 사용하여 Anc80 캡시드 단백질을 함유하는 AAV 내로 패키징될 수 있다. 바이러스 입자의 성분 (예를 들어, rep 서열, cap 서열, 역전된 말단 반복부 (ITR) 서열)은 본원에 기재된 바와 같은 1개 이상의 구축물을 사용하여 패키징 숙주 세포 내로 일시적으로 또는 안정하게 도입될 수 있다. 관심 폴리뉴클레오티드는 일반적으로 큰 유전자 (예를 들어, 4 kB 이상)일 수 있으며, 이는 1개 초과의 AAV 내로 분할 및 패키징되는 것이 요구될 수 있다.
일부 실시양태에서, AAV9-php.b 벡터를 함유하는 AAV는 내이 세포를 효율적으로 표적화하는 데 사용될 수 있다. AAV9-php.b는 국제 공개 번호 WO 2019/173367 (PCT/US2019/020794)에 기재되어 있으며, 이의 내용은 그 전문이 본원에 참조로 포함된다. AAV-PHP.B는 7-량체 서열 TLAVPFK (서열식별번호: 59)를 코딩하고, 트랜스진을 와우로 효율적으로 전달하며, 여기서 이는 내유모 및 외유모 세포에서 현저하게 특이적이고 강건한 발현을 나타냈다. AAV-PHP.B 벡터는 본원에 기재된 프로모터 중 임의의 것을 포함할 수 있지만 이에 제한되지는 않는다.
폴리뉴클레오티드 요법 방법에 사용하기 위한 cDNA 발현은 임의의 적합한 프로모터 (예를 들어, 인간 시토메갈로바이러스 (CMV), 원숭이 바이러스 40 (SV40) 또는 메탈로티오네인 프로모터)로부터 지시되고, 임의의 적절한 포유동물 조절 요소에 의해 조절될 수 있다. 예를 들어, 원하는 경우에, 특정 세포 유형에서 유전자 발현을 우선적으로 지시하는 것으로 공지된 인핸서가 핵산의 발현을 지시하는 데 사용될 수 있다. 사용되는 인핸서는 비제한적으로 조직- 또는 세포-특이적 인핸서로서 특징화되는 것을 포함할 수 있다. 대안적으로, 게놈 클론이 치료 구축물로서 사용되는 경우에, 조절은 동족 조절 서열에 의해 매개될 수 있거나, 또는 원하는 경우에, 상기 기재된 임의의 프로모터 또는 조절 요소를 포함한, 이종 공급원으로부터 유래된 조절 서열에 의해 매개될 수 있다.
치료 방법
본 개시내용에 포함된 또 다른 치료 접근법은 재조합 치료제 (예를 들어, 재조합 STRC 단백질, 그의 변이체 또는 단편)를 잠재적 또는 실제 질환-이환 조직의 부위에 직접적으로 또는 전신으로 (예를 들어, 임의의 통상적인 재조합 단백질 투여 기술에 의해) 투여하는 것을 수반할 수 있다. 투여되는 단백질의 투여량은 개별 환자의 크기 및 건강을 포함한 다수의 인자에 좌우된다. 임의의 특정한 대상체의 경우, 구체적 투여 요법은 개체 필요에 따라 및 조성물을 투여하거나 투여를 감독하는 사람의 전문적 판단에 따라 시간 경과에 따라 조정되어야 한다.
본 개시내용의 일부 실시양태는 세포 (예를 들어, 대상체의 세포) (여기서 세포의 게놈은 돌연변이를 포함할 수 있음)에서 전장 관심 단백질 (예를 들어, STRC)을 코딩하는 뉴클레오티드 서열을 함유하는 벡터 시스템 (예를 들어, 이중-벡터 인테인-매개 시스템)을 포함하는 제약 조성물의 치료 유효량을 투여하는 것을 포함하는, 질환 및/또는 장애 또는 그의 증상의 치료 또는 예방 또는 감소를 필요로 하는 대상체에서 질환 및/또는 장애 또는 그의 증상을 치료 또는 예방 또는 감소시키는 방법을 제공할 수 있다. 본 개시내용의 이중-벡터 인테인-매개 시스템을 사용하는 실시양태에서, 질환 및/또는 장애 또는 그의 증상의 치료 또는 예방 또는 감소를 필요로 하는 대상체에서 질환 및/또는 장애 또는 그의 증상을 치료 또는 예방 또는 감소시키는 방법은, 그를 필요로 하는 대상체 (여기서 대상체는, 예를 들어 포유동물, 예컨대 인간임)에서 돌연변이를 포함하는 게놈에 관심 단백질의 부분 (예를 들어, N-STRC)을 코딩하는 제1 뉴클레오티드 서열 및 관심 단백질의 나머지 부분 (예를 들어, C-STRC)을 코딩하는 제2 뉴클레오티드 서열을 함유하는 이중-벡터 인테인-매개 시스템을 포함하는 제약 조성물의 치료 유효량을 투여하는 것을 포함할 수 있다. 따라서, 한 실시양태는 돌연변이와 연관된 질환 또는 장애 또는 그의 증상을 앓고 있거나 그에 걸리기 쉬운 대상체를 치료하는 방법이다. 방법은 대상체에게 질환 또는 장애 또는 증상을 치료 또는 예방 또는 감소시키기에 충분한 치료량의 본원의 조성물을 투여하는 것을 포함한다. 일부 실시양태에서, 돌연변이는 열성 돌연변이이다.
본 발명의 치료 방법 (이는 예방적 치료를 포함함)은 일반적으로 그를 필요로 하는 포유동물, 예를 들어 인간을 포함한 대상체 (예를 들어, 동물, 인간)에게 치료 유효량의 본원의 화합물 또는 조성물, 예컨대 본원의 화학식의 화합물을 투여하는 것을 포함한다. 이러한 치료는 질환, 장애 또는 그의 증상을 앓고 있거나, 그를 갖거나, 그에 걸리기 쉽거나 또는 그의 위험이 있는 대상체, 특히 인간에게 적합하게 투여될 것이다. "위험이 있는" 대상체의 결정은 대상체 또는 건강 관리 제공자의 진단 검사 또는 의견 (예를 들어, 유전자 검사, 효소 또는 단백질 마커, 마커 (본원에 정의된 바와 같음), 가족력 등)에 의한 임의의 객관적 또는 주관적 결정에 의해 이루어질 수 있다.
인간 환자 또는 비-인간 동물의 치료는 생리학상 허용되는 담체 중 치료 유효량의 조합 치료제를 사용하여 수행될 수 있다. 어구 "제약상 허용되는"은 타당한 의학적 판단의 범주 내에서, 합리적인 이익/위험 비에 상응하게, 과도한 독성, 자극, 알레르기 반응 또는 다른 문제 또는 합병증 없이 인간 및 동물의 조직과 접촉하여 사용하기에 적합한 본 개시내용의 화합물, 이러한 화합물을 함유하는 조성물 및/또는 투여 형태를 지칭한다.
조성물은 편리하게는 단위 투여 형태로 제공될 수 있고, 관련 기술분야에 널리 공지된 임의의 방법에 의해 제조될 수 있다. 단일 투여 형태를 생산하기 위해 담체 물질과 조합될 수 있는 조성물 (예를 들어, 관심 단백질 (예를 들어, STRC)의 N-말단 또는 C-말단 부분을 코딩하는 서열을 함유하는 벡터)의 양은 치료될 숙주, 특정한 투여 방식에 따라 달라질 것이다. 담체 물질과 조합되어 단일 투여 형태를 생성할 수 있는 조성물의 양은 일반적으로 치료 효과를 생성하는 조성물의 양일 것이다. 일반적으로, 100 퍼센트 중, 이 양은 조성물의 1% 내지 99% (예를 들어, 5%-70%, 10%-30%)의 범위일 것이다.
조성물은 질환 또는 상태의 임상 또는 생리학적 증상을 제어하는 투여량으로 투여될 수 있으며, 이는 일부 경우에 관련 기술분야의 통상의 기술자에게 공지된 진단 방법에 의해 결정될 수 있다.
치료 조성물 및 치료 조합물은 유효량으로 투여된다. 예를 들어, 약 108 내지 약 1012 바이러스 입자가 대상체에게 투여될 수 있고, 바이러스는 적합한 부피 (예를 들어, 10 μL, 50 μL, 100 μL, 500 μL 또는 1000 μL)의, 예를 들어 인공 외림프 용액 중에 현탁될 수 있다.
상염색체 열성 청력 상실을 치료하는 방법
상염색체 열성 청력 상실 (예를 들어, 난청, 상염색체 열성 16의 비-증후군성 난청 (DFNB16))을 치료하기 위한 조성물 및 방법이 제공된다.
간략하게, DFNB16은 이환된 개체의 STRC 유전자 내의 돌연변이와 연관된다. 내이 내, 스테레오실린 (STRC) 세포외 구조 단백질을 코딩하는 STRC의 정상 발현은 청각 기능에 필수적이다. 청력 상실의 회복을 유도하기 위해, 야생형 STRC 유전자는 본원에 기재된 바와 같은 벡터 시스템 (예를 들어, 이중-AAV 인테인-매개 STRC 단백질 트랜스-스플라이싱 시스템)을 사용하여, 즉 전장 mRNA 및 전장 STRC 단백질이 발현되도록 야생형 STRC 유전자 서열 또는 그의 단편을 패키징함으로써 대상체에게 투여된다.
일부 실시양태에서, 예를 들어 이중-AAV 인테인-매개 STRC 단백질 트랜스-스플라이싱 벡터를 포함한 STRC 단백질을 코딩하는 벡터 시스템은 스테레오실린 (STRC) 단백질을 코딩하는 적어도 1개의 벡터 (예를 들어, 5' STRC 및 3' STRC 벡터)를 대상체의 와우 내로 직접 주사함으로써 DFNB16 청력 상실을 갖는 대상체에게 투여될 수 있다. 일부 실시양태에서, 1개의 벡터는 N-STRC 단백질만을 코딩하고, 1개의 벡터는 C-STRC 단백질만을 코딩한다. 치료 목적을 위해, STRC 폴리펩티드 또는 STRC 폴리펩티드를 코딩하는 STRC 폴리뉴클레오티드를 포함하는 조성물은 질환 또는 상태에 의해 이환된 신체 영역 (예를 들어, 와우)에 직접 투여될 수 있으며, 여기서 대상체의 게놈은 본원에 기재된 바와 같은 청력 상실 (예를 들어, DFNB16)을 유발하거나 또는 이에 기여하는 STRC 돌연변이를 포함한다.
한 실시양태는 상염색체 열성 청력 상실의 치료를 필요로 하는 대상체에게 유효량의 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템); 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템)을 함유하는 세포; 또는 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템) 및 제약상 허용되는 비히클을 포함하는 제약 조성물을 투여하는 것을 포함하는, 대상체에서 상염색체 열성 청력 상실을 치료하는 방법을 제공할 수 있다. 일부 실시양태는 DFNB16인 상염색체 열성 청력 상실을 치료하는 방법에 관한 것일 수 있다.
본 개시내용의 또 다른 실시양태는 대상체의 세포를 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템) 및 제약상 허용되는 비히클을 포함하는 조성물과 접촉시키는 것을 포함하며, 여기서 접촉시키는 것은 단백질의 N-말단 부분을 발현하는 제1 뉴클레오티드 서열 및 단백질의 C-말단 부분을 발현하는 제2 뉴클레오티드 서열의 세포 내로의 전달을 일으키고, 여기서 세포는 펩티드 결합에 의해 연결된 단백질의 N-말단 부분 및 단백질의 C-말단 부분을 발현하여 전장 단백질을 형성하는 것인 방법을 제공한다.
본 개시내용의 추가 실시양태는 청력 상실을 특징으로 하는 병리상태 또는 질환의 치료 및/또는 예방을 필요로 하는 대상체에게 유효량의 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템); 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템)을 함유하는 세포; 또는 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템) 및 제약상 허용되는 비히클을 포함하는 제약 조성물을 투여하는 것을 포함하며, 여기서 투여 단계는 대상체의 적어도 1개의 세포 (예를 들어, 내이 세포, 내유모 세포, 외유모 세포)에서 이루어지는 것인, 청력 상실을 특징으로 하는 병리상태 또는 질환을 치료 및/또는 예방하는 방법을 제공한다. 한 실시양태에서, 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템); 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템)을 함유하는 세포; 또는 본원에 기재된 벡터 시스템 (예를 들어, 이중-벡터 시스템) 및 제약상 허용되는 비히클을 포함하는 제약 조성물의 유효량을 세포와 접촉시키거나 또는 세포에 투여하는 방법은 생체내, 생체외 및/또는 시험관내에서 이루어진다. 또 다른 실시양태는 본원에 기재된 임의의 방법을 제공하며, 여기서 방법은 대상체에서 청각 기능을 개선 또는 회복시킨다.
비제한적 투여 방법은 와우관 또는 와우관 주위의 외림프-충전된 공간 (예를 들어, 고실계 및 전정계) 내로 주사하는 것을 포함할 수 있다. 고칼륨 내림프액으로 충전된 와우관 내로의 주사는 유모 세포에 대한 직접적 접근을 제공할 수 있다. 그러나, 이러한 섬세한 유체 환경에 대한 변경은 와우내 잠재력을 파괴하여, 주사-관련 독성에 대한 위험을 높일 수 있다. 와우관을 둘러싸는 외림프-충전된 공간, 고실계 및 전정계는 난원창 또는 원형창 막을 통해 중이로부터 접근될 수 있다. 내이 내로의 유일한 비-골성 개구부인 원형창 막은 많은 동물 모델에서 비교적 용이하게 접근가능하고, 이 경로를 사용한 바이러스 벡터의 투여는 잘 허용된다. 인간에서, 와우 이식물 배치는 상용적으로 원형창 막을 통한 외과적 전극 삽입에 의존한다.
일부 실시양태에서, 관심 단백질 (예를 들어, 야생형 STRC)을 발현하는 것은 대상체에서 청각 기능을 회복시킬 수 있다. 일부 실시양태에서, 대상체에게 회복된 청각 기능은 10% 이상 (예를 들어, 20%, 30%, 40%, 50%, 60%, 70%, 80%, 90%, 100%); 100% 이하 (예를 들어, 95%, 85%, 75%, 65%, 55%, 45%, 35%, 25%, 15%)일 수 있다.
실시예
하기 실시예는 본 설명의 구체적 측면을 예시한다. 실시예는 단지 실시양태 및 그의 다양한 측면의 구체적 이해 및 실시를 제공하기 때문에, 실시예는 제한적인 것으로 해석되어서는 안된다.
실시예 1: 이중-벡터 시스템은 시험관내에서 큰 유전자를 형질도입한다
AAV 벡터 생산
본원에 개시된 관심 단백질의 전달을 위한 이중-벡터 또는 이중-트랜스-스플라이싱 시스템을, 예를 들어 내이 내로의 2개의 독립적 아데노-연관 바이러스, 혈청형 2 (AAV2)/아데노-연관 바이러스, 혈청형 9 (AAV9)-Php.B 벡터에서의 STRC 코딩 서열을 사용하여 입증하였다. STRC 코딩 서열의 처음 2,247개 염기 쌍 (즉, STRC의 N-말단 부분) 바로 뒤에 위치하고 3'-ITR이 이어지는 스플라이스 공여자 서열 (예를 들어, N-인테인)을 갖는 제1 AAV 게놈을 생산하였다 (예를 들어, AAV2/AAV9-Php.B-STRC-trans/공여자). 5'-ITR 뒤에 및 나머지 STRC 코딩 서열 (즉, STRC의 C-말단 부분) (C-말단 myc 태그를 가짐) 바로 앞에 위치하는 상응하는 스플라이스 수용자 서열을 갖는 제2 AAV 게놈을 생산하였다 (예를 들어, AAV2/AAV9-Php.B-STRC-trans/수용자). AAV2 게놈은 바이러스 게놈의 각각의 말단에 역전된 말단 반복부 (ITR)를 갖는 콘카테머를 형성하는 것으로 공지되어 있기 때문에, STRC 코딩 서열을 2개의 단편으로 나누고, 개별 AAV 캡시드 (예를 들어, 합성 AAV: 효율적으로 내유모 및 외유모 세포를 형질도입시키는 것으로 제시된 Anc80) 내로 패키징하였다.
인테인-매개 트랜스-스플라이싱 및 프로세싱을 확인하기 위해, 전장 STRC의 부분을 코딩하는 AAV2/AAV9-Php.B 벡터로 감염된 HEK293 세포 (감염 5일 후)를 웨스턴 블롯에 의해 분석하였다 (도 24). 구체적으로, 도 24는 하기를 보여준다: 레인 1: 대조군 또는 형질감염되지 않은 HEK293T 세포; 레인 2: 전장 스테레오실린 (STRC) (196.4 kDa); 레인 3: pCFS-#2, C 부분 (C-부분 (116.7 kDa)만을 갖는 구축물 #2가 있는 벡터); 레인 4: pCFS-#2, N+C 부분 (N- 및 C-부분을 갖는 구축물 #2가 있는 벡터); 레인 5: pCFS-#1, C 부분 (C-부분 (91.6 kDa)만을 갖는 구축물 #1이 있는 벡터); 레인 6: pCFS-#1, N+C 부분 (N- 및 C-부분을 갖는 구축물 #1이 있는 벡터). 웨스턴 블롯의 우측 화살표는 레인 4에서의 전장 STRC 단백질을 가리키며, 이는 STRC의 N-말단 부분 및 C-말단 부분을 코딩하는 서열을 각각 함유하는 2개의 AAV2/AAV9-Php.B 벡터가 HEK293 세포 내로 형질감염되었을 때 STRC의 N-말단 부분 및 C-말단 부분 둘 다가 형성되었다는 것을 입증한다.
신호 서열의 유용성을 확인하기 위해, 추가의 웨스턴 블롯을 수행하였다. 도 25는 하기를 보여준다: 레인 1: 전장 스테레오실린 (STRC) (196.4 kDa); 레인 2: 대조군 또는 형질감염되지 않은 HEK293T 세포; 레인 3: pCFS-#2, C 부분, (-) 신호 (신호 서열이 없는 C-부분 (116.7 kDa)만을 갖는 구축물 #2가 있는 벡터); 레인 4: pCFS-#2, N+C 부분, (-) 신호 (신호 서열이 없는 N- 및 C-부분을 갖는 구축물 #2가 있는 벡터); 레인 5: pCFS-#2, C 부분, (+) 신호 (신호 서열이 있는 C-부분 (91.6 kDa)만을 갖는 구축물 #2가 있는 벡터); 레인 6: pCFS-#2, N+C 부분, (+) 신호 (신호 서열이 있는 N- 및 C-부분을 갖는 구축물 #2가 있는 벡터). 웨스턴 블롯의 우측의 화살표는 레인 6에서의 전장 STRC 단백질을 가리키며, 이는 신호 서열이 전장 STRC 단백질의 형성을 일으키는 데 필요하였다는 것을 입증한다.
AAV 벡터는 보스턴 아동 병원 바이러스 코어(Boston Children's Hospital Viral Core) (미국 매사추세츠주 보스턴)에 의해 생산되었다. STRC 및 인테인을 함유하는 플라스미드를 AAV9-php.b-cmv 내로의 패키징 (MGH DNA 코어, 완전 플라스미드 서열분석) 전에 서열분석하였다. 벡터 역가는 바이러스의 역전된 말단 반복부 (AAV2)에 특이적인 qPCR에 의해 결정 시 4.8x1014 gc/ml였다.
실시예 2: 생체내 Strc 녹아웃 마우스에서의 이중-벡터 시스템의 분석
동물
모든 동물을 사육하고, 시설에 수용하였다. 동물을 수반하는 모든 연구는 동물에 대한 HMS 상설 위원회 (프로토콜 번호 03524) 및 보스턴 아동 병원 동물 실험 윤리 위원회 (프로토콜 번호 2878 및 3396)에 의해 승인되었다. 모든 실험을 동물 프로토콜에 따라 수행하였다.
스테레오실린 결핍인 널 대립유전자 ("녹아웃") 마우스 (STRC-/-; StrcΔ/Δ)를 생성하고, 부재하는 또는 비-기능적 스테레오실린 단백질을 유도하는 STRC 돌연변이에 의해 유발된 인간 청력 상실 DFNB16 표현형에 대한 마우스 모델로서 제공하였다. Strc 동형접합 돌연변이 마우스 (STRC#16 homo)는 청각 뇌간 반응 (ABR)에 의해 결정 시 4주령까지 중증 청력 상실을 나타냈고, 6주령까지 돌연변이 마우스는 완전히 사망하였다. Strc 동형접합 돌연변이 마우스는 또한 최대 80 dB 음압 수준의 검출가능한 변조 이음향방사 (DPOAE)가 결여되었으며, 이는 정상 외유모 세포 (OHC) 기능의 부재를 반영한다.
StrcΔ/Δ 마우스를 생성하고, 도 32a-32g에서 특징화하였다. 야생형 (WT) 관심 단백질, 예를 들어 Strc를, Strc 유전자의 엑손 4를 표적화하도록 3개의 가이드 RNA (sgRNA)를 설계함으로써 CRISPR/Cas9 전략을 사용하여 파괴하였다. 파괴는 249개의 뉴클레오티드 결실 (위치 1509-1758) 및 2개의 전위 및 역위 (3' 말단에 보다 가까운 위치 947-1139; 5' 말단에 보다 가까운 위치 1758-1835)를 생성하였다.
내이 주사
생후 제1일 (P1)에 Strc-/- 또는 StrcWT/WT 마우스 새끼의 내이에 1 μl의 AAV9-php.b-cmv-STRC 인테인 바이러스를 60 nl/분의 속도로 주사하였다. 새끼를 2-3분 동안 빙수에서 저체온 노출을 사용하여 마취시켰다. 마취 시, 귀-후방부 절개를 수행하여 귀 수포를 노출시키고 와우를 가시화하였다. 유리 마이크로피펫에 의해 수동으로 주사하였다. 주사 후, 봉합사를 사용하여 피부 절단부를 봉합하였다. 이어서, 주사된 마우스를 회복시키기 위해 42℃ 가열 패드 상에 두었다. 새끼가 ~10분 내에 완전히 회복된 후에 어미에게 돌려보냈다. 수술 후에 표준 수술후 관리를 적용하였다. 생체내 연구를 위한 샘플 크기를 계속적으로 결정하여 샘플 크기를 최적화하고 분산을 감소시켰다. P5 내지 P7에, 주사된 귀로부터 코르티 기관을 절제하였다. 코르티 기관 조직을 37℃, 5% CO2에서 8-10일 동안 인큐베이션하고, 전기생리학 기록 직전에 덮개막을 제거하였다.
청력 검사
각각 N-인테인을 갖는 N-STRC 및 C-인테인을 갖는 C-STRC를 코딩하는 서열을 포함하는 AAV 벡터를 사용한 이중-벡터 시스템이 청력 상실을 회복시킬 수 있는지 여부 및 회복시키는 정도를 결정하기 위해, 스테레오실린 녹아웃 (STRC-/-) 마우스에서 청각 뇌간 반응 (ABR) 및 변조 이음향방사 (DPOAE)를 측정하였다. EPL 음향 시스템 (매사추세츠 아이 앤드 이어(Massachusetts Eye and Ear), 보스턴)을 사용하여 ABR 및 DPOAE 측정을 기록하였다. 음향 자극을 PXI-1042Q 섀시에서 24-비트 디지털 입력/출력 카드 (내셔널 인스트루먼츠(National Instruments) PXI-4461)로 생성하고, SA-1 스피커 드라이버 (터커-데이비스 테크놀로지스, 인크.(Tucker-Davis Technologies, Inc.))에 의해 증폭시키고, 맞춤 음향 시스템에서 2개의 정전기적 드라이버 (CUI CDMG15008-03A)로부터 전달하였다. 작은 프로브 튜브 말단의 일렉트렛 마이크로폰 (놀스(Knowles) FG-23329-P07)을 사용하여 이도 음압을 모니터링하였다. 동일한 세션 동안 마우스로부터 ABR 및 DPOAE를 기록하였다. 귓바퀴 (활동 전극), 두정 (기준 전극) 및 둔부 (접지 전극)에 삽입된 피하 바늘 전극을 사용하여 ABR 신호를 수집하였다. ABR 전위를 증폭시키고 (10,000x), 통과-여과시키고 (0.3-10 kHz), 이튼-피바디 래보러토리즈(Eaton-Peabody Laboratories)의 와우 기능 검사 모음으부터의 맞춤 데이터 획득 소프트웨어 (랩뷰(LabVIEW))를 사용하여 디지털화하였다. 소리 자극 및 전극 전압을 디지털 I-O 보드 (내셔널 인스트루먼츠)를 사용하여 40-μs 간격으로 샘플링하고, 오프라인 분석을 위해 저장하였다. 역치는 시각적으로 피크 1이 검출될 수 있고 소리 강도를 증가시킴에 따라 재현될 수 있는 최저 데시벨 수준으로 정의하였다. ABR 역치를 각각의 실험군 내에서 평균내고, 통계적 분석에 사용하였다. 유전자형에 대해 맹검인 조사자에 의해 ABR 및 DPOAE 측정을 수행하였다.
마우스를 크실라진 (5-10 mg/kg) 및 케타민 (60-100 mg/kg)의 복강내 (i.p.) 주사로 마취시키고, 귓바퀴의 기저부를 잘라내어 이도를 노출시켰다. a) 양쪽 귀 사이의 등쪽 (기준 전극); b) 왼쪽 귓바퀴 뒤쪽 (기록 전극); 및 c) 동물의 둔부의 등쪽 (접지 전극)을 비롯하여, 피부 내로 3개의 피하 바늘 전극을 삽입하였다. 세션 전반에 걸쳐 필요한 경우 마취를 유지하기 위해 케타민의 추가의 분취물 (60-100 mg/kg i.p.)을 제공하였다. ABR 시험 전에, 모든 자극 주파수에서 각각의 개별 시험 대상체에 대해 이도의 입구에서의 음압을 보정하였다. ABR 및 DPOAE 데이터를 동일한 조건 하에 및 동일한 기록 세션 동안 수집하였다.
DPOAE를 먼저 기록하였다. 2f1-f2에서의 DPOAE를 생성하기 위해 1.2의 주파수 비 (f1 및 f2 1차 음의 주파수 비 (f2/f1 = 1.2))로 1차 음을 생성하였으며, 여기서 f2 수준은 각각의 f2/f1 쌍에 대해 f1 수준 미만의 10 dB 음압 수준이었다. 음을 1/2-옥타브 단계에서 5.6 내지 32.0 kHz로 달라지는 f2 및 L1-L2 = 10 데시벨 음압 수준 (dB SPL)으로 제시하였다. 각각의 f2에서, L2를 10 dB 증분으로 10 내지 80 dB로 변동시켰다. DPOAE 역치는 평균 스펙트럼으로부터 잡음 플로어보다 5 dB 높은 크기의 DPOAE를 도출하는 L2-수준으로 정의하였다. 평균 잡음 플로어 수준은 모든 주파수에 걸쳐 0 dB 미만이었다. 각각의 수준에서, 기록된 이도 음압의 신호-대-잡음 (s/n) 비를 증가시키기 위해 파형 및 스펙트럼 평균을 사용하였다. 2f1-f2에서의 DPOAE는 평균낸 스펙트럼으로부터 추출된 진폭, 뿐만 아니라 스펙트럼 내의 이웃 지점에서의 잡음 플로어를 가졌다. DPOAE 진폭 대 소리 수준의 플롯으로부터의 내삽은 이소-반응 곡선을 생성하였다. 역치는 0 dB 초과의 DPOAE를 생성하는 데 요구되는 f2 수준으로 정의하였다.
이어서, 방음 챔버 내 32℃에서 ABR 실험을 수행하였다. 청각 기능을 시험하기 위해, 마우스에게 반-옥타브 단계로 5.6 내지 32.0 kHz의 광대역 "클릭" 음뿐만 아니라 순수 음의 자극을 제시하였고, 모두 5-ms 음 삐소리로 제시하였다. 반응을 증폭시키고 (10,000회), 여과하고 (0.1-3 kHz), PC-기반 데이터-획득 시스템 (EPL, 와우 기능 검사 모음, MEE, 보스턴)에서 아날로그-대-디지털 보드로 평균내었다. 다양한 시험에 걸쳐, 소리 수준을 5 내지 10 dB 단계로 0에서 110 dB SPL로 상승시켰다. 각각의 수준에서, 512개의 반응을 수집하고, "인공물 거부" 후에 각각의 음압 수준 (자극 극성이 교대됨)에 대해 평균내었다. 배경 잡음 대비 피크 1의 출현의 육안 검사에 의해 역치를 결정하였다. 오리진-2015 (오리진랩 코포레이션(OriginLab Corporation), 매사추세츠주)를 사용하여 데이터를 분석하고 플롯팅하였다. 달리 언급되지 않는 한 역치 평균 ± 표준 편차가 제시된다. 이들 실험의 대다수를 맹검 조건 하에 수행하지 않았다.
NHEJ-매개 Cas9-생성된 절단에 의해 Strc 유전자 코딩 서열을 파괴함으로써 STRC가 결여된 녹아웃 마우스를 생성하였다. STRC 유전자의 엑손 4 내에 ~200개 염기 쌍 결실을 생성하였으며, 이는 기능적 단백질의 합성을 방해하였다. 이러한 마우스 모델은 부재하는 또는 비-기능적 스테레오실린 단백질을 생성하는 STRC 돌연변이에 의해 유발된 DFNB16 표현형의 인간 청력 상실을 정확하게 재현하는 것으로 밝혀졌다. 제4주 연령의 STRC 동형접합 돌연변이 마우스는 청각 뇌간 반응 (ABR)에 기초하여 중증 청력 상실을 나타냈고, 제6주까지 이들 마우스는 완전히 사망하였다. ABR 역치는 명확한 반응 (CR)이 존재하는 최저 수준일 수 있다. 변조 이음향방사 (DPOAE)는 외유모 세포 완전성 및 와우 기능을 반영한다. 이들 STRC 동형접합 돌연변이 마우스는 또한 최대 80 데시벨 (dB) 음압 수준의 검출가능한 DPOAE를 가졌으며, 이는 정상 외유모 세포 (OHC) 기능의 부재를 반영한다.
도 3은 ABR 파형 결과로부터의 음압 수준을 보여준다. 중앙 및 좌측 파형은 각각 STRC KO 마우스, STRC-/- 마우스, (Strc#16 homo) 단독 (n=5) 및 AAV 벡터를 포함하는 본원에 기재된 이중-벡터 시스템 (여기서 각각의 AAV 벡터는 신호 서열, N-인테인 또는 C-인테인 및 STRC 단백질의 N-말단 또는 C-말단 부분을 코딩하는 서열을 함유함) (예를 들어, AAV2/AAV9-Php.B-Cmv-Strc-N; AAV2/AAV9-Php.B-Cmv-Strc-C)이 주사된 마우스 (n=9)의 결과를 보여주며, 우측 파형은 무손상 STRC 유전자를 갖는 야생형 (WT) 마우스 (STRCWT/WT) (n=6)를 나타낸다. WT 마우스는 30 dB 내지 100 dB 범위의 음압 수준을 나타냈다. 중앙의 STRC KO 마우스 (Strc#16 homo)는 70 dB 내지 120 dB 범위의 제한된 음압 수준을 나타냈으며, 이는 70 dB 미만의 청력 상실을 입증한다. 그러나, 좌측 파형은 AAV2/AAV9-Php.B-Cmv-Strc-N; AAV2/AAV9-Php.B-Cmv-Strc-C가 주사된 STRC KO 마우스가 WT STRC 마우스의 것에 상응하는 수준으로 청력 상실을 회복할 수 있었다는 것을 입증한다.
평균 청력 역치 또는 ABR을 4-주령 마우스에서 모든 주파수에 걸쳐 시험하였다. 도 4a의 ABR 결과는 AAV 벡터를 포함하는 본원에 기재된 이중-벡터 시스템 (여기서 각각의 AAV 벡터는 각각 신호 서열, N-인테인 또는 C-인테인 및 STRC 단백질의 N-말단 또는 C-말단 부분을 코딩하는 서열을 함유함) (예를 들어, AAV2/AAV9-Php.B-Cmv-Strc-N; AAV2/AAV9-Php.B-Cmv-Strc-C)이 각각 주사된 STRC 녹아웃 (KO) 마우스 (Strc-/-) (n=9; 중간선)가 최저 ABR 역치가 일부 주파수에서 30 dB만큼 낮아져 청력 상실의 회복을 입증하였다는 것을 보여주었다. 야생형 마우스 (n=6; 가장 하부의 선)로부터의 ABR 반응은 최저 ABR 역치가 일부 주파수에서 20 dB만큼 낮아졌다. 그러나, STRC KO 마우스 (n=5; 상부 선)는 역치가 80 dB 초과로 중증 청력 상실을 가졌다.
도 5a 및 도 6a에서의 ABR 결과는 역치가 80 dB 초과인 중증 청력 상실을 갖는 STRC KO 마우스 (n=5; 상부 선과 오차 막대)를 보여준다. N-STRC (n=4; AAV2/AAV9-Php.B-Cmv-Strc-N) 또는 C-STRC (n=3; AAV2/AAV9-Php.B-Cmv-Strc-C)를 코딩하는 야생형 STRC의 부분을 코딩하는 인테인 AAV 중 어느 하나가 주사된 STRC KO 마우스는 STRC KO 마우스 결과와 유사한, 즉 80 dB 초과의 청력 역치를 나타냈다. 그러나, 야생형 마우스 (n=5; 가장 하부의 선)로부터의 ABR 반응은 최저 ABR 역치가 일부 주파수에서 20 dB만큼 낮아졌다.
도 4b의 DPOAE 결과 (도 45a에 사용된 동일한 STRC KO 마우스를 사용함)는 AAV 벡터를 포함하는 본원에 기재된 이중-벡터 시스템 (여기서 각각의 AAV 벡터는 신호 서열, N-인테인 또는 C-인테인 및 STRC 단백질의 N-말단 또는 C-말단 부분을 코딩하는 서열을 함유함) (예를 들어, 각각 AAV2/AAV9-Php.B-Cmv-Strc-N; AAV2/AAV9-Php.B-Cmv-Strc-C; n=9; 중간선)이 주사된 STRC KO 마우스가 일부 주파수에서 30 dB만큼 낮아진 DPOAE 반응에 의해 입증된 바와 같이 청력 상실의 회복을 나타냈다는 것을 입증하였다. 유사하게, 야생형 마우스 (n=6; 가장 하부의 선)는 최저 DPOAE 역치가 일부 주파수에서 30 dB만큼 낮아진 DPOAE 반응을 나타냈다. 그러나, STRC KO 마우스 (n=5; 상부 선)는 시험된 조건 (최대 80 dB) 하에 어떠한 DPOAE 반응도 나타내지 않았다.
도 5b 및 도 6b의 DPOAE 결과 (도 5a 및 6a에 사용된 동일한 STRC KO 마우스를 사용함)는 STRC KO 마우스 (n=5; 상부 선)가 시험된 조건 (최대 80 dB) 하에 어떠한 DPOAE 반응도 나타내지 않았다는 것을 입증하였다. 유사하게, N-STRC (n=4; AAV2/AAV9-Php.B-Cmv-Strc-N) 또는 C-STRC (n=3; AAV2/AAV9-Php.B-Cmv-Strc-C)를 코딩하는 야생형 STRC의 부분을 코딩하는 인테인 AAV 중 어느 하나가 주사된 STRC KO 마우스는 어떠한 DPOAE 반응도 나타내지 않았다. 그러나, 야생형 마우스 (n=5; 가장 하부의 선)는 최저 DPOAE 역치가 일부 주파수에서 30 dB만큼 낮아진 DPOAE 반응을 나타냈다.
도 7a 및 7b는 AAV 벡터를 포함하는 본원에 기재된 이중-벡터 시스템 (여기서 각각의 AAV 벡터는 신호 서열, N-인테인 또는 C-인테인 및 STRC 단백질의 N-말단 또는 C-말단 부분을 코딩하는 서열을 함유함) (예를 들어, 각각 AAV2/AAV9-Php.B-Cmv-Strc-N; AAV2/AAV9-Php.B-Cmv-Strc-C)이 주사된 3마리의 STRC KO 마우스의 시간 경과에 따른 모니터링 결과를 입증한다. 각각의 마우스에 대한 ABR 반응은 일반적으로 4주에서 마우스에 대해 일부 주파수에서 최저 역치를 보여주었다 (실선). 일반적으로, 각각의 마우스에 대해 시간 경과에 따라, 역치는 4주에서 달성된 것과 비교하여 6주 (파선) 및 8주 (파선/점선)에서 증가하였다. 예를 들어, 도 7a는 4주 (실선)에서, 마우스 #3이 10 kHz 미만의 주파수에서 40 dB 내지 55 dB 범위의 ABR 역치를 가졌고, 6주 (파선)에서, 마우스 #3이 10 kHz 미만의 주파수에서 50 dB 내지 70 dB 범위의 ABR 역치를 가졌으며, 이는 4주에서 관찰된 것보다 더 큰 데시벨이었다는 것을 보여준다. DPOAE 반응의 경우, 시간 경과에 따라 더 낮은 주파수로부터 더 높은 주파수로의 이동이 관찰되었다. 도 7b에서, 가낭 낮은 DPOAE 역치 반응 (50 dB)은 마우스 #3에 대해 4주에서 11 kHz의 주파수 및 6주에서 16 kHz에서 발생하였다.
실시예 3: 이중-벡터 시스템을 사용한 형태의 회복
이중 AAV 전달 시스템은 알렉사488 접합된 2차 항체 (녹색) 및 알렉사546-팔로이딘 (적색)을 갖는 항-STRC 항체로 염색된 와우의 시각적 관찰에 의해 입증된 바와 같이 STRC 발현 및 유모 다발 형태를 회복시켰다. 예를 들어, 도 33a는 야생형 (WT) Strc 또는 StrcΔ/Δ가 주사된 와우 및 이중 AAV 벡터 주사된 StrcΔ/Δ 와우의 공초점 영상을 제시한다. STRC 및 액틴을 염색하였으며, WT (상부 좌측)에서는 둘 다 관찰되었고, StrcΔ/Δ + 이중 AAV 벡터 샘플 (상부 우측)에서는 부분적으로 관찰된 반면, StrcΔ/Δ (상부 중간)에서는 파괴된 액틴 외유모 세포 (OHC) 다발이 관찰되었다. WT에서의 녹색 염색 및 역전된 V 유모 다발의 형성 (하부 좌측) 및 StrcΔ/Δ + 이중 AAV 벡터 샘플에서의 부분적 제시 또는 회복 (하부 우측)에 의해 STRC 국재화가 제시되었고, StrcΔ/Δ는 어떠한 녹색 염색된 유모 다발 (하부 중앙)도 나타내지 않았다.
스캐닝 전자 현미경검사 영상에서 본 개시내용의 이중 AAV 벡터 전달 시스템이 도 33b의 유모 다발 형태 (하단 패널)를 거의 WT 수준 (상단 패널)으로 회복시키는 것으로 관찰되었다. StrcΔ/Δ 주사된 외유모 세포 다발은 야생형의 조직화된 OHC 다발과 대조적으로 비배열 또는 비조직화된 OHC 다발 (중간 패널)을 생성한다.
실시예 4: 이중-벡터 시스템을 사용한 청각 기능의 회복
이중 AAV 벡터 시스템은 또한 음압 수준 10 dB 내지 50 dB 범위의 DPOAE 파형의 푸리에 분석에 의해 입증된 바와 같이 DPOAE 및 ABR 역치를 회복시켰으며, 여기서 StrcΔ/Δ + 이중 AAV 벡터 샘플 (도 34a, 우측)은 야생형 (도 34a, 좌측)의 경우와 유사한 청각 기능 패턴을 갖는 것으로 관찰되었고, DPOAE 역치는 이중 AAV 벡터 주사된 StrcΔ/Δ 마우스가 청각 기능을 회복시켰음을 나타낸다 (도 34b). 야생형 (도 34c, 좌측) 및 StrcΔ/Δ + 이중 AAV 벡터 (도 34c, 우측) 주사된 와우에 대해 기록된 ABR 트레이스는 25 dB 내지 110 dB 범위의 유사한 음압 수준을 유발한 반면; StrcΔ/Δ 주사된 와우의 경우 70 dB 내지 120 dB의 음압 수준을 유발하였다 (도 34c, 중간). ABR 역치는 마우스에게 StrcΔ/Δ 단독과 비교하여 StrcΔ/Δ + 이중 AAV 벡터를 주사한 경우에 5 kHz 내지 30 kHz 범위의 주파수에서 회복을 입증하는 것으로 나타났다 (도 34d).
구체적 실시양태
비제한적 구체적 실시양태가 하기 기재되며, 이들 각각은 본 개시내용 내에 있는 것으로 간주된다.
구체적 실시양태 1. 세포에서 관심 단백질을 발현시키기 위한 이중-벡터 시스템이며,
a) 5'에서 3' 방향으로:
- 관심 단백질의 아미노 말단 (N-말단) 부분을 코딩하는 부분 코딩 서열의 5'-말단에 있는 신호 서열;
- 관심 단백질의 N-말단 부분을 코딩하는 부분 코딩 서열;
- 부분 코딩 서열에 인접하고 그의 하류인 스플라이스 공여자 서열을 코딩하는 서열
을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터; 및
b) 5'에서 3' 방향으로:
- 관심 단백질의 카르복시 말단 (C-말단) 부분을 코딩하는 부분 코딩 서열의 5'-말단에 있는 신호 서열;
- 신호 서열 및 관심 단백질의 C-말단 부분을 코딩하는 부분 코딩 서열이 플랭킹된 스플라이스 수용자 서열을 코딩하는 서열;
- 관심 단백질의 C-말단 부분을 코딩하는 부분 코딩 서열
을 포함하는 제2 뉴클레오티드 서열을 포함하는 제2 벡터
를 포함하는 이중-벡터 시스템.
구체적 실시양태 2. 구체적 실시양태 1에 있어서,
a) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 관심 단백질의 아미노 말단 (N-말단) 부분을 코딩하는 부분 코딩 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 인테인의 아미노 말단 단편 (N-인테인)을 코딩하는 서열;
- 폴리-아데닐화 (폴리A) 신호 서열;
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터; 및
b) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 인테인의 카르복시 말단 단편 (C-인테인)을 코딩하는 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 관심 단백질의 카르복시 말단 (C-말단) 부분을 코딩하는 부분 코딩 서열;
- 폴리-아데닐화 (폴리A) 신호 서열;
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제2 뉴클레오티드 서열을 포함하는 제2 벡터
를 포함하는 이중-벡터 시스템.
구체적 실시양태 3. 구체적 실시양태 1 또는 2에 있어서, 세포에서 제1 벡터 및 제2 벡터가 각각
a) N-말단에서 C-말단 방향으로:
- 신호 펩티드 서열, 이에 연결된 관심 단백질 서열의 N-말단 부분, 이의 C-말단 단부에서 융합된 N-인테인 단백질 서열
을 포함하는 제1 단백질 서열; 및
b) N-말단에서 C-말단 방향으로:
- 신호 펩티드 서열, 이에 연결된 C-인테인 단백질 서열, 이에 N-말단 단부가 융합된 관심 단백질 서열의 C-말단 부분
을 포함하는 제2 단백질 서열
을 발현하는 것인 이중-벡터 시스템.
구체적 실시양태 4. 구체적 실시양태 1-3 중 어느 하나에 있어서, 관심 단백질의 N-말단 부분 및 관심 단백질의 C-말단 부분이 전장 관심 단백질을 형성하도록 구성된 것인 이중-벡터 시스템.
구체적 실시양태 5. 구체적 실시양태 1-4 중 어느 하나에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 동일한 것인 이중-벡터 시스템.
구체적 실시양태 6. 구체적 실시양태 1-4 중 어느 하나에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 제1 단백질 서열 및 제2 단백질 서열을 동일한 세포 구획으로 수송하도록 구성된 것인 이중-벡터 시스템.
구체적 실시양태 7. 구체적 실시양태 1-4 중 어느 하나에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 상이하고, 각각의 신호 펩티드 서열이 각각의 단백질 서열을 동일한 세포 구획으로 지시하는 것인 이중-벡터 시스템.
구체적 실시양태 8. 구체적 실시양태 1-7 중 어느 하나에 있어서, 제1 벡터 및 제2 벡터가 각각 바이러스 벡터인 이중-벡터 시스템.
구체적 실시양태 9. 구체적 실시양태 8에 있어서, 바이러스 벡터가 아데노-연관 바이러스 (AAV) 벡터인 이중-벡터 시스템.
구체적 실시양태 10. 구체적 실시양태 8 또는 구체적 실시양태 9에 있어서, 바이러스 벡터가 동일하거나 상이한 혈청형인 이중-벡터 시스템.
구체적 실시양태 11. 구체적 실시양태 1-10 중 어느 하나에 있어서, N-말단 부분 및 C-말단 부분이 펩티드 결합을 통해 전장 관심 단백질을 형성하도록 구성된 것인 이중-벡터 시스템.
구체적 실시양태 12. 구체적 실시양태 1-11 중 어느 하나에 있어서, 관심 단백질이 STRC 단백질인 이중-벡터 시스템.
구체적 실시양태 13. 구체적 실시양태 12에 있어서, STRC 단백질이 STRC 유전자에 의해 코딩되는 것인 이중-벡터 시스템.
구체적 실시양태 14. 구체적 실시양태 1-13 중 어느 하나에 있어서, 신호 서열이 서열식별번호: 9 또는 서열식별번호: 11에 대해 적어도 80% 동일성 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 15. 구체적 실시양태 1-14 중 어느 하나에 있어서, 신호 서열이 서열식별번호: 10 또는 서열식별번호: 12에 대해 적어도 80% 동일성 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 갖는 신호 펩티드 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 16. 구체적 실시양태 1-15 중 어느 하나에 있어서, 관심 단백질의 N-말단 부분이 서열식별번호: 5 또는 서열식별번호: 7에 대해 또는 서열식별번호: 15 또는 서열식별번호: 16을 코딩하는 핵산 서열에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 17. 구체적 실시양태 1-16 중 어느 하나에 있어서, 관심 단백질의 N-말단 부분이 서열식별번호: 15 또는 서열식별번호: 16에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 18. 구체적 실시양태 1-17 중 어느 하나에 있어서, N-인테인 서열이 서열식별번호: 13에 대해 적어도 80% 동일성 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 19. 구체적 실시양태 1-18 중 어느 하나에 있어서, N-인테인 서열이 서열식별번호: 14에 대해 적어도 80% 동일성 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 20. 구체적 실시양태 1-19 중 어느 하나에 있어서, 관심 단백질의 C-말단 부분이 서열식별번호: 23 또는 서열식별번호: 24를 코딩하는 핵산 서열에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 21. 구체적 실시양태 1-20 중 어느 하나에 있어서, 관심 단백질의 C-말단 부분이 서열식별번호: 23 또는 서열식별번호: 24에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 22. 구체적 실시양태 1-21 중 어느 하나에 있어서, C-인테인 서열이 서열식별번호: 21 또는 서열식별번호: 46에 대해 적어도 80% 동일성 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 23. 구체적 실시양태 1-22 중 어느 하나에 있어서, C-인테인 서열이 서열식별번호: 22 또는 서열식별번호: 49에 대해 적어도 80% 동일성 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 24. 구체적 실시양태 1-23 중 어느 하나에 있어서, 제1 뉴클레오티드 서열이 서열식별번호: 5 또는 서열식별번호: 7에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 25. 구체적 실시양태 1-24 중 어느 하나에 있어서, 제1 뉴클레오티드 서열이 서열식별번호: 6 또는 서열식별번호: 8에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 26. 구체적 실시양태 1-25 중 어느 하나에 있어서, 제2 뉴클레오티드 서열이 서열식별번호: 17 또는 서열식별번호: 19에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 27. 구체적 실시양태 1-26 중 어느 하나에 있어서, 제2 뉴클레오티드 서열이 서열식별번호: 18 또는 서열식별번호: 20에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 28. 숙주 세포에서 STRC 유전자의 코딩 서열을 발현시키기 위한 벡터 시스템이며, 여기서 코딩 서열은 서열식별번호: 1, 서열식별번호: 3, 서열식별번호: 5, 서열식별번호: 7, 서열식별번호: 17, 서열식별번호: 19, 서열식별번호: 29, 서열식별번호: 31, 서열식별번호: 33 또는 서열식별번호: 38의 STRC 유전자, 서열식별번호: 30 또는 서열식별번호: 32의 mRNA 서열 또는 그의 단편을 포함하는 적어도 1개의 벡터를 포함하는 것인 벡터 시스템.
구체적 실시양태 29. 구체적 실시양태 28에 있어서, STRC 유전자가 서열식별번호: 2, 서열식별번호: 4, 서열식별번호: 6, 서열식별번호: 8, 서열식별번호: 15, 서열식별번호: 16, 서열식별번호: 18, 서열식별번호: 20, 서열식별번호: 23, 서열식별번호: 24, 서열식별번호: 25, 서열식별번호: 26, 서열식별번호: 36 또는 서열식별번호: 39 또는 그의 조합의 STRC 단백질을 코딩하는 것인 벡터 시스템.
구체적 실시양태 30. 구체적 실시양태 28에 있어서, 숙주 세포에서 STRC 유전자의 코딩 서열을 발현시키기 위한 이중-벡터 시스템을 포함하며, 여기서 코딩 서열은 5' 말단 단편 및 3' 말단 단편을 포함하고, 이중-벡터 시스템은
a) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, STRC 유전자 코딩 서열의 5' 말단 단편;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 인테인의 아미노 말단 단편 (N-인테인)을 코딩하는 서열;
- 폴리-아데닐화 (폴리A) 신호 서열; 및
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터; 및
b) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 인테인의 카르복시 말단 단편 (C-인테인)을 코딩하는 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, STRC 유전자 코딩 서열의 3' 말단 단편;
- 폴리-아데닐화 (폴리A) 신호 서열; 및
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제2 뉴클레오티드 서열을 포함하는 제2 벡터
를 포함하는 것인 벡터 시스템.
구체적 실시양태 31. 구체적 실시양태 30에 있어서, 세포에서 제1 벡터 및 제2 벡터가 각각
a) N-말단에서 C-말단 방향으로:
- 신호 펩티드 서열, 이에 연결된 STRC 단백질 서열의 N-말단 부분, 이의 C-말단 단부에서 융합된 N-인테인 단백질 서열
을 포함하는 제1 단백질 서열; 및
b) N-말단에서 C-말단 방향으로:
- 신호 펩티드 서열, 이에 연결된 C-인테인 단백질 서열, 이에 N-말단 단부가 융합된 STRC 단백질 서열의 C-말단 부분
을 포함하는 제2 단백질 서열
을 발현하는 것인 이중-벡터 시스템.
구체적 실시양태 32. 구체적 실시양태 30-31 중 어느 하나에 있어서, STRC 단백질의 N-말단 부분 및 STRC 단백질의 C-말단 부분이 전장 STRC 단백질을 형성하는 것인 이중-벡터 시스템.
구체적 실시양태 33. 구체적 실시양태 30-32 중 어느 하나에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 동일한 것인 이중-벡터 시스템.
구체적 실시양태 34. 구체적 실시양태 30-33 중 어느 하나에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 제1 단백질 서열 및 제2 단백질 서열을 동일한 세포 구획으로 수송하도록 구성된 것인 이중-벡터 시스템.
구체적 실시양태 35. 구체적 실시양태 30-34 중 어느 하나에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 상이하고, 각각의 신호 펩티드 서열이 각각의 단백질 서열을 동일한 세포 구획으로 지시하는 것인 이중-벡터 시스템.
구체적 실시양태 36. 구체적 실시양태 30-35 중 어느 하나에 있어서, 제1 벡터 및 제2 벡터가 각각 바이러스 벡터인 이중-벡터 시스템.
구체적 실시양태 37. 구체적 실시양태 36에 있어서, 바이러스 벡터가 아데노-연관 바이러스 (AAV) 벡터인 이중-벡터 시스템.
구체적 실시양태 38. 구체적 실시양태 36 또는 구체적 실시양태 37에 있어서, 바이러스 벡터가 동일한 혈청형을 갖는 것인 이중-벡터 시스템.
구체적 실시양태 39. 구체적 실시양태 36 또는 구체적 실시양태 37에 있어서, 바이러스 벡터가 상이한 혈청형을 갖는 것인 이중-벡터 시스템.
구체적 실시양태 40. 구체적 실시양태 30-39 중 어느 하나에 있어서, N-말단 부분 및 C-말단 부분이 펩티드 결합을 통해 전장 STRC 단백질을 형성하는 것인 이중-벡터 시스템.
구체적 실시양태 41. 구체적 실시양태 30-40 중 어느 하나에 있어서, STRC 단백질이 STRC 유전자에 의해 코딩되는 것인 이중-벡터 시스템.
구체적 실시양태 42. 구체적 실시양태 30-41 중 어느 하나에 있어서, 신호 서열이 서열식별번호: 9 또는 서열식별번호: 11에 대해 적어도 80% 동일성 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 43. 구체적 실시양태 30-42 중 어느 하나에 있어서, 신호 서열이 서열식별번호: 10 또는 서열식별번호: 12에 대해 적어도 80% 동일성 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 44. 구체적 실시양태 30-43 중 어느 하나에 있어서, STRC 단백질의 N-말단 부분이 서열식별번호: 5 또는 서열식별번호: 7에 대해 또는 서열식별번호: 15 또는 서열식별번호: 16을 코딩하는 핵산 서열에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 45. 구체적 실시양태 30-44 중 어느 하나에 있어서, STRC 단백질의 N-말단 부분이 서열식별번호: 6, 서열식별번호: 8, 서열식별번호: 15 또는 서열식별번호: 16에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 46. 구체적 실시양태 30-45 중 어느 하나에 있어서, STRC 단백질의 N-말단 부분이 전장 STRC 단백질의 N-말단 단부 부분의 54% 미만 (예를 들어, 53.8%, 53.6%, 53.4%, 53.2%, 53%, 52%, 50%, 45%)을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 47. 구체적 실시양태 30-46 중 어느 하나에 있어서, N-인테인 서열이 서열식별번호: 13에 대해 적어도 80% 동일성 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 48. 구체적 실시양태 30-47 중 어느 하나에 있어서, N-인테인 서열이 서열식별번호: 14에 대해 적어도 80% 동일성 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 49. 구체적 실시양태 30-48 중 어느 하나에 있어서, STRC 단백질의 C-말단 부분이 서열식별번호: 17, 서열식별번호: 19에 대해 또는 서열식별번호: 18, 서열식별번호: 20, 서열식별번호: 23 또는 서열식별번호: 24를 코딩하는 핵산 서열에 대해 적어도 70% (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%) 동일성의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 50. 구체적 실시양태 30-49 중 어느 하나에 있어서, STRC 단백질의 C-말단 부분이 서열식별번호: 18, 서열식별번호: 20, 서열식별번호: 23 또는 서열식별번호: 24에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 51. 구체적 실시양태 30-50 중 어느 하나에 있어서, STRC 단백질의 C-말단 부분이 전장 STRC 단백질의 C-말단 단부 부분의 46% 이상 (예를 들어, 46.2%, 46.4%, 46.6%, 46.8%, 47%, 48%, 50%, 55%)을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 52. 구체적 실시양태 30-51 중 어느 하나에 있어서, C-인테인 서열이 서열식별번호: 21에 대해 적어도 80% 동일한 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%) 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 53. 구체적 실시양태 30-52 중 어느 하나에 있어서, C-인테인 서열이 서열식별번호: 22에 대해 적어도 80% 동일한 (예를 들어, 85%, 90%, 95%, 96%, 97%, 98%, 99%) 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 54. 구체적 실시양태 30-53 중 어느 하나에 있어서, 제1 뉴클레오티드 서열이 서열식별번호: 5 또는 서열식별번호: 7에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 55. 구체적 실시양태 30-54 중 어느 하나에 있어서, 제1 뉴클레오티드 서열이 서열식별번호: 6, 서열식별번호: 8, 서열식별번호: 15 또는 서열식별번호: 16에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 56. 구체적 실시양태 30-55 중 어느 하나에 있어서, 제2 뉴클레오티드 서열이 서열식별번호: 17 또는 서열식별번호: 19에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 핵산 서열을 포함하는 것인 이중-벡터 시스템.
구체적 실시양태 57. 구체적 실시양태 30-56 중 어느 하나에 있어서, 제2 뉴클레오티드 서열이 서열식별번호: 18, 서열식별번호: 20, 서열식별번호: 23 또는 서열식별번호: 24에 대해 적어도 70% 동일성 (예를 들어, 75%, 80%, 85%, 90%, 95%, 96%, 97%, 98%, 99%)의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
구체적 실시양태 58. 구체적 실시양태 1-57 중 어느 하나의 벡터 시스템을 함유하는 적어도 1개의 세포 (예를 들어, 10, 20, 50, 100, 200, 500, 1000개 또는 생물학적 활성을 갖는 큰 단백질을 성공적으로 발현하기에 충분한 임의의 개수의 세포)이며, 대상체에서 상염색체 열성 청력 상실일 수 있는 청력 상실을 치료, 억제 또는 감소시키기 위한 것일 수 있는 적어도 1개의 세포.
구체적 실시양태 59. 대상체에서 상염색체 열성 청력 상실일 수 있는 청력 상실을 치료, 억제 또는 감소시키기 위한, 구체적 실시양태 1-57 중 어느 하나의 벡터 시스템 및 제약상 허용되는 비히클을 포함하는 제약 조성물.
구체적 실시양태 60. 상염색체 열성 청력 상실의 치료, 억제 또는 감소를 필요로 하는 대상체에게 유효량의 구체적 실시양태 1-57 중 어느 하나의 이중-벡터 시스템을 투여하는 것을 포함하는, 대상체에서 상염색체 열성 청력 상실을 치료, 억제 또는 감소시키는 방법.
구체적 실시양태 61. 상염색체 열성 청력 상실의 치료, 억제 또는 감소를 필요로 하는 대상체에게 유효량의 구체적 실시양태 58의 적어도 1개의 세포를 투여하는 것을 포함하는, 대상체에서 상염색체 열성 청력 상실을 치료, 억제 또는 감소시키는 방법.
구체적 실시양태 62. 상염색체 열성 청력 상실의 치료, 억제 또는 감소를 필요로 하는 대상체에게 유효량의 구체적 실시양태 59의 제약 조성물을 투여하는 것을 포함하는, 대상체에서 상염색체 열성 청력 상실을 치료, 억제 또는 감소시키는 방법.
구체적 실시양태 63. 구체적 실시양태 60-62 중 어느 하나에 있어서, 상염색체 열성 청력 상실이 DFNB16인 방법.
구체적 실시양태 64. 대상체의 적어도 1개의 세포를 구체적 실시양태 59의 제약 조성물과 접촉시키는 것을 포함하는 방법이며, 여기서 접촉은 제1 뉴클레오티드 서열 및 제2 뉴클레오티드 서열을 포함하는 벡터 시스템을 대상체의 적어도 1개의 세포 내로 전달하고, 여기서 접촉된 적어도 1개의 세포는 펩티드 결합에 의해 연결된 단백질의 N-말단 부분 및 단백질의 C-말단 부분을 발현하여 전장 단백질을 형성하는 것인 방법.
구체적 실시양태 65. 청력 상실을 특징으로 하는 병리상태 또는 질환의 치료 및/또는 예방을 필요로 하는 대상체에게 유효량의 구체적 실시양태 1-57 중 어느 하나에 따른 벡터 시스템, 구체적 실시양태 58에 따른 적어도 1개의 세포 또는 구체적 실시양태 59에 따른 제약 조성물을 투여하는 것을 포함하는, 청력 상실을 특징으로 하는 병리상태 또는 질환을 치료 및/또는 예방하는 방법.
구체적 실시양태 66. 구체적 실시양태 64-65 중 어느 하나에 있어서, 적어도 1개의 세포가 내이 세포인 방법.
구체적 실시양태 67. 구체적 실시양태 64-66 중 어느 하나에 있어서, 적어도 1개의 세포가 내유모 세포 또는 외유모 세포인 방법.
구체적 실시양태 68. 구체적 실시양태 60-67 중 어느 하나에 있어서, 적어도 1개의 세포가 생체내 또는 시험관내 세포인 방법.
구체적 실시양태 69. 구체적 실시양태 60-68 중 어느 하나에 있어서, 대상체에서 청각 기능을 개선 또는 회복시키는 방법.
상기 기재로부터, 본원에 기재된 본 발명을 다양한 용법 및 조건에 채택하기 위해 그에 대해 변경 및 변형이 이루어질 수 있다는 것이 분명할 것이다. 이러한 실시양태는 또한 하기 청구범위의 범주 내에 있다.
본원의 변수의 임의의 정의에서 요소의 목록의 언급은 열거된 요소의 임의의 단일 요소 또는 조합 (또는 하위조합)으로서의 그 변수의 정의를 포함한다. 본원의 실시양태의 언급은 그 실시양태를 임의의 단일 실시양태로서 또는 임의의 다른 실시양태 또는 그의 부분과 조합하여 포함한다.
본 명세서에서 언급된 모든 특허 및 간행물은 각각의 독립적인 특허 및 간행물이 구체적으로 및 개별적으로 참조로 포함되는 것으로 나타내어진 것과 동일한 정도로 그 전문이 본원에 참조로 포함된다.
SEQUENCE LISTING
<110> THE CHILDREN'S MEDICAL CENTER CORPORATION
<120> LARGE GENE VECTORS AND DELIVERY AND USES THEREOF
<130> 167705.020601/PCT
<140> PCT/US2021/016720
<141> 2021-02-05
<150> 62/971,555
<151> 2020-02-07
<160> 63
<170> PatentIn version 3.5
<210> 1
<211> 5262
<212> DNA
<213> Homo sapiens
<400> 1
gtgactctgg cccctactgg gcctcattcc ctggaccctg gtctctcctt cctgaagtca 60
ttgctctcca ctctggacca ggctccccag ggctccctga gccgctcacg gttctttaca 120
ttcctggcca acatttcttc ttcctttgag cctgggagaa tgggggaagg accagtagga 180
gagcccccac ctctccagcc gcctgctctg cggctccatg attttctagt gacactgaga 240
ggtagccccg actgggagcc aatgctaggg ctgctagggg atatgctggc actgctggga 300
caggagcaga ctccccgaga tttcctggtg caccaggcag gggtgctggg tggacttgtg 360
gaggtgctgc tgggagcctt agttcctggg ggccccccta ccccaactcg gcccccatgc 420
acccgtgatg ggccgtctga ctgtgtcctg gctgctgact ggttgccttc tctgctgctg 480
ttgttagagg gcacacgctg gcaagctctg gtgcaggtgc agcccagtgt ggaccccacc 540
aatgccacag gcctcgatgg gagggaggca gctcctcact ttttgcaggg tctgttgggt 600
ttgcttaccc caacagggga gctaggctcc aaggaggctc tttggggcgg tctgctacgc 660
acagtggggg cccccctcta tgctgccttt caggaggggc tgctccgtgt cactcactcc 720
ctgcaggatg aggtcttctc cattttgggg cagccagagc ctgataccaa tgggcagtgc 780
cagggaggta accttcaaca gctgctctta tggggcgtcc ggcacaacct ttcctgggat 840
gtccaggcgc tgggctttct gtctggatca ccacccccac cccctgccct ccttcactgc 900
ctgagcacgg gcgtgcctct gcccagagct tctcagccgt cagcccacat cagcccacgc 960
caacggcgag ccatcactgt ggaggccctc tgtgagaacc acttaggccc agcaccaccc 1020
tacagcattt ccaacttctc catccacttg ctctgccagc acaccaagcc tgccactcca 1080
cagccccatc ccagcaccac tgccatctgc cagacagctg tgtggtatgc agtgtcctgg 1140
gcaccaggtg cccaaggctg gctacaggcc tgccacgacc agtttcctga tgagtttttg 1200
gatgcgatct gcagtaacct ctccttttca gccctgtctg gctccaaccg ccgcctggtg 1260
aagcggctct gtgctggcct gctcccaccc cctaccagct gccctgaagg cctgccccct 1320
gttcccctca ccccagacat cttttggggc tgcttcttgg agaatgagac tctgtgggct 1380
gagcgactgt gtggggaggc aagtctacag gctgtgcccc ccagcaacca ggcttgggtc 1440
cagcatgtgt gccagggccc caccccagat gtcactgcct ccccaccatg ccacattgga 1500
ccctgtgggg aacgctgccc ggatgggggc agcttcctgg tgatggtctg tgccaatgac 1560
accatgtatg aggtcctggt gcccttctgg ccttggctag caggccaatg caggataagt 1620
cgtgggggca atgacacttg cttcctagaa gggctgctgg gcccccttct gccctctctg 1680
ccaccactgg gaccatcccc actctgtctg acccctggcc ccttcctcct tggcatgcta 1740
tcccagttgc cacgctgtca gtcctctgtc ccagctcttg ctcaccccac acgcctacac 1800
tatctcctcc gcctgctgac cttcctcttg ggtccagggg ctgggggcgc tgaggcccag 1860
gggatgctgg gtcgggccct actgctctcc agtctcccag acaactgctc cttctgggat 1920
gcctttcgcc cagagggccg gcgcagtgtg ctacggacga ttggggaata cctggaacaa 1980
gatgaggagc agccaacccc atcaggcttt gaacccactg tcaaccccag ctctggtata 2040
agcaagatgg agctgctggc ctgctttagt cctgtgctgt gggatctgct ccagagggaa 2100
aagagtgttt gggccctgca gattctagtg caggcgtacc tgcatatgcc cccagaaaac 2160
ctccagcagc tggtgctttc agcagagagg gaggctgcac agggcttcct gacactcatg 2220
ctgcagggga agctgcaggg gaagctgcag gtaccaccat ccgaggagca ggccctgggt 2280
cgcctgacag ccctgctgct ccagcggtac ccacgcctca cctcccagct cttcattgac 2340
ctgtcaccac tcatcccttt cttggctgtc tctgacctga tgcgcttccc accatccctg 2400
ttagccaacg acagtgtcct ggctgccatc cgggattaca gcccaggaat gaggcctgaa 2460
cagaaggagg ctctggcaaa gcgactgctg gcccctgaac tgtttgggga agtgcctgcc 2520
tggccccagg agctgctgtg ggcagtgctg cccctgctcc cccacctccc tctggagaac 2580
tttttgcagc tcagccctca ccagatccag gccctggagg atagctggcc agcagcaggt 2640
ctggggccag ggcatgcccg ccatgtgctg cgcagcctgg taaaccagag tgtccaggat 2700
ggtgaggagc aggtacgcag gcttgggccc ctcgcctgtt tcctgagccc tgaggagctg 2760
cagagcctag tgcccctgag tgatccaacg gggccagtag aacgggggct gctggaatgt 2820
gcagccaatg ggaccctcag cccagaagga cgggtggcat atgaacttct gggtgtgttg 2880
cgctcatctg gaggagcggt gctgagcccc cgggagctgc gggtctgggc ccctctcttc 2940
tctcagctgg gcctccgctt ccttcaggag ctgtcagagc cccagcttag agccatgctt 3000
cctgtcctgc agggaactag tgttacacct gctcaggctg tcctgctgct tggacggctc 3060
cttcctaggc acgatctatc cctggaggaa ctctgctcct tgcaccttct gctaccaggc 3120
ctcagccccc agacactcca ggccatccct aggcgagtcc tggtcggggc ttgttcctgc 3180
ctggcccctg aactgtcacg cctctcagcc tgccagaccg cagcactgct gcagaccttt 3240
cgggttaaag atggtgttaa aaatatgggt acaacaggtg ctggtccagc tgtgtgtatc 3300
cctggtcagc ctattcccac cacctggcca gactgcctgc ttcccctgct cccattaaag 3360
ctgctacaac tggattcctt ggctcttctg gcaaatcgaa gacgctactg ggagctgccc 3420
tggtctgagc agcaggcaca gtttctctgg aagaagatgc aagtacccac caaccttacc 3480
ctcaggaatc tgcaggctct gggcaccctg gcaggaggca tgtcctgtga gtttctgcag 3540
cagatcaact ccatggtaga cttccttgaa gtggtgcaca tgatctatca gctgcccact 3600
agagttcgag ggagcctgag ggcctgtatc tgggcagagc tacagcggag gatggcaatg 3660
ccagaaccag aatggacaac tgtagggcca gaactgaacg ggctggatag caagctactc 3720
ctggacttac cgatccagtt gatggacaga ctatccaatg aatccattat gttggtggtg 3780
gagctggtgc aaagagctcc agagcagctg ctggcactga cccccctcca ccaggcagcc 3840
ctggcagaga gggcactaca aaacctggct ccaaaggaga ctccagtctc aggggaagtg 3900
ctggagacct taggcccttt ggttggattc ctggggacag agagcacacg acagatcccc 3960
ctacagatcc tgctgtccca tctcagtcag ctgcaaggct tctgcctagg agagacattt 4020
gccacagagc tgggatggct gctattgcag gagtctgttc ttgggaaacc agagttgtgg 4080
agccaggatg aagtagagca agctggacgc ctagtattca ctctgtctac tgaggcaatt 4140
tccttgatcc ccagggaggc cttgggtcca gagaccctgg agcggcttct agaaaagcag 4200
cagagctggg agcagagcag agttggacag ctgtgtaggg agccacagct tgctgccaag 4260
aaagcagccc tggtagcagg ggtggtgcga ccagctgctg aggatcttcc agaacctgtg 4320
ccaaattgtg cagatgtacg agggacattc ccagcagcct ggtctgcaac ccagattgca 4380
gagatggagc tctcagactt tgaggactgc ctgacattat ttgcaggaga cccaggactt 4440
gggcctgagg aactgcgggc agccatgggc aaagcaaaac agttgtgggg tcccccccgg 4500
ggatttcgtc ctgagcagat cctgcagctt ggtaggctct taataggtct aggagatcgg 4560
gaactacagg agctgatcct agtggactgg ggagtgctga gcaccctggg gcagatagat 4620
ggctggagca ccactcagct ccgcattgtg gtctccagtt tcctacggca gagtggtcgg 4680
catgtgagcc acctggactt cgttcatctg acagcgctgg gttatactct ctgtggactg 4740
cggccagagg agctccagca catcagcagt tgggagttca gccaagcagc tctcttcctc 4800
ggcaccctgc atctccagtg ctctgaggaa caactggagg ttctggccca cctacttgta 4860
ctgcctggtg ggtttggccc aatcagtaac tgggggcctg agatcttcac tgaaattggc 4920
accatagcag ctgggatccc agacctggct ctttcagcac tgctgcgggg acagatccag 4980
ggcgttactc ctcttgccat ttctgtcatc cctcctccta aatttgctgt ggtgtttagt 5040
cccatccaac tatctagtct caccagtgct caggctgtgg ctgtcactcc tgagcaaatg 5100
gcctttctga gtcctgagca gcgacgagca gttgcatggg cccaacatga gggaaaggag 5160
agcccagaac agcaaggtcg aagtacagcc tggggcctcc aggactggtc acgaccttcc 5220
tggtccctgg tattgactat cagcttcctt ggccacctgc ta 5262
<210> 2
<211> 1754
<212> PRT
<213> Homo sapiens
<400> 2
Val Thr Leu Ala Pro Thr Gly Pro His Ser Leu Asp Pro Gly Leu Ser
1 5 10 15
Phe Leu Lys Ser Leu Leu Ser Thr Leu Asp Gln Ala Pro Gln Gly Ser
20 25 30
Leu Ser Arg Ser Arg Phe Phe Thr Phe Leu Ala Asn Ile Ser Ser Ser
35 40 45
Phe Glu Pro Gly Arg Met Gly Glu Gly Pro Val Gly Glu Pro Pro Pro
50 55 60
Leu Gln Pro Pro Ala Leu Arg Leu His Asp Phe Leu Val Thr Leu Arg
65 70 75 80
Gly Ser Pro Asp Trp Glu Pro Met Leu Gly Leu Leu Gly Asp Met Leu
85 90 95
Ala Leu Leu Gly Gln Glu Gln Thr Pro Arg Asp Phe Leu Val His Gln
100 105 110
Ala Gly Val Leu Gly Gly Leu Val Glu Val Leu Leu Gly Ala Leu Val
115 120 125
Pro Gly Gly Pro Pro Thr Pro Thr Arg Pro Pro Cys Thr Arg Asp Gly
130 135 140
Pro Ser Asp Cys Val Leu Ala Ala Asp Trp Leu Pro Ser Leu Leu Leu
145 150 155 160
Leu Leu Glu Gly Thr Arg Trp Gln Ala Leu Val Gln Val Gln Pro Ser
165 170 175
Val Asp Pro Thr Asn Ala Thr Gly Leu Asp Gly Arg Glu Ala Ala Pro
180 185 190
His Phe Leu Gln Gly Leu Leu Gly Leu Leu Thr Pro Thr Gly Glu Leu
195 200 205
Gly Ser Lys Glu Ala Leu Trp Gly Gly Leu Leu Arg Thr Val Gly Ala
210 215 220
Pro Leu Tyr Ala Ala Phe Gln Glu Gly Leu Leu Arg Val Thr His Ser
225 230 235 240
Leu Gln Asp Glu Val Phe Ser Ile Leu Gly Gln Pro Glu Pro Asp Thr
245 250 255
Asn Gly Gln Cys Gln Gly Gly Asn Leu Gln Gln Leu Leu Leu Trp Gly
260 265 270
Val Arg His Asn Leu Ser Trp Asp Val Gln Ala Leu Gly Phe Leu Ser
275 280 285
Gly Ser Pro Pro Pro Pro Pro Ala Leu Leu His Cys Leu Ser Thr Gly
290 295 300
Val Pro Leu Pro Arg Ala Ser Gln Pro Ser Ala His Ile Ser Pro Arg
305 310 315 320
Gln Arg Arg Ala Ile Thr Val Glu Ala Leu Cys Glu Asn His Leu Gly
325 330 335
Pro Ala Pro Pro Tyr Ser Ile Ser Asn Phe Ser Ile His Leu Leu Cys
340 345 350
Gln His Thr Lys Pro Ala Thr Pro Gln Pro His Pro Ser Thr Thr Ala
355 360 365
Ile Cys Gln Thr Ala Val Trp Tyr Ala Val Ser Trp Ala Pro Gly Ala
370 375 380
Gln Gly Trp Leu Gln Ala Cys His Asp Gln Phe Pro Asp Glu Phe Leu
385 390 395 400
Asp Ala Ile Cys Ser Asn Leu Ser Phe Ser Ala Leu Ser Gly Ser Asn
405 410 415
Arg Arg Leu Val Lys Arg Leu Cys Ala Gly Leu Leu Pro Pro Pro Thr
420 425 430
Ser Cys Pro Glu Gly Leu Pro Pro Val Pro Leu Thr Pro Asp Ile Phe
435 440 445
Trp Gly Cys Phe Leu Glu Asn Glu Thr Leu Trp Ala Glu Arg Leu Cys
450 455 460
Gly Glu Ala Ser Leu Gln Ala Val Pro Pro Ser Asn Gln Ala Trp Val
465 470 475 480
Gln His Val Cys Gln Gly Pro Thr Pro Asp Val Thr Ala Ser Pro Pro
485 490 495
Cys His Ile Gly Pro Cys Gly Glu Arg Cys Pro Asp Gly Gly Ser Phe
500 505 510
Leu Val Met Val Cys Ala Asn Asp Thr Met Tyr Glu Val Leu Val Pro
515 520 525
Phe Trp Pro Trp Leu Ala Gly Gln Cys Arg Ile Ser Arg Gly Gly Asn
530 535 540
Asp Thr Cys Phe Leu Glu Gly Leu Leu Gly Pro Leu Leu Pro Ser Leu
545 550 555 560
Pro Pro Leu Gly Pro Ser Pro Leu Cys Leu Thr Pro Gly Pro Phe Leu
565 570 575
Leu Gly Met Leu Ser Gln Leu Pro Arg Cys Gln Ser Ser Val Pro Ala
580 585 590
Leu Ala His Pro Thr Arg Leu His Tyr Leu Leu Arg Leu Leu Thr Phe
595 600 605
Leu Leu Gly Pro Gly Ala Gly Gly Ala Glu Ala Gln Gly Met Leu Gly
610 615 620
Arg Ala Leu Leu Leu Ser Ser Leu Pro Asp Asn Cys Ser Phe Trp Asp
625 630 635 640
Ala Phe Arg Pro Glu Gly Arg Arg Ser Val Leu Arg Thr Ile Gly Glu
645 650 655
Tyr Leu Glu Gln Asp Glu Glu Gln Pro Thr Pro Ser Gly Phe Glu Pro
660 665 670
Thr Val Asn Pro Ser Ser Gly Ile Ser Lys Met Glu Leu Leu Ala Cys
675 680 685
Phe Ser Pro Val Leu Trp Asp Leu Leu Gln Arg Glu Lys Ser Val Trp
690 695 700
Ala Leu Gln Ile Leu Val Gln Ala Tyr Leu His Met Pro Pro Glu Asn
705 710 715 720
Leu Gln Gln Leu Val Leu Ser Ala Glu Arg Glu Ala Ala Gln Gly Phe
725 730 735
Leu Thr Leu Met Leu Gln Gly Lys Leu Gln Gly Lys Leu Gln Val Pro
740 745 750
Pro Ser Glu Glu Gln Ala Leu Gly Arg Leu Thr Ala Leu Leu Leu Gln
755 760 765
Arg Tyr Pro Arg Leu Thr Ser Gln Leu Phe Ile Asp Leu Ser Pro Leu
770 775 780
Ile Pro Phe Leu Ala Val Ser Asp Leu Met Arg Phe Pro Pro Ser Leu
785 790 795 800
Leu Ala Asn Asp Ser Val Leu Ala Ala Ile Arg Asp Tyr Ser Pro Gly
805 810 815
Met Arg Pro Glu Gln Lys Glu Ala Leu Ala Lys Arg Leu Leu Ala Pro
820 825 830
Glu Leu Phe Gly Glu Val Pro Ala Trp Pro Gln Glu Leu Leu Trp Ala
835 840 845
Val Leu Pro Leu Leu Pro His Leu Pro Leu Glu Asn Phe Leu Gln Leu
850 855 860
Ser Pro His Gln Ile Gln Ala Leu Glu Asp Ser Trp Pro Ala Ala Gly
865 870 875 880
Leu Gly Pro Gly His Ala Arg His Val Leu Arg Ser Leu Val Asn Gln
885 890 895
Ser Val Gln Asp Gly Glu Glu Gln Val Arg Arg Leu Gly Pro Leu Ala
900 905 910
Cys Phe Leu Ser Pro Glu Glu Leu Gln Ser Leu Val Pro Leu Ser Asp
915 920 925
Pro Thr Gly Pro Val Glu Arg Gly Leu Leu Glu Cys Ala Ala Asn Gly
930 935 940
Thr Leu Ser Pro Glu Gly Arg Val Ala Tyr Glu Leu Leu Gly Val Leu
945 950 955 960
Arg Ser Ser Gly Gly Ala Val Leu Ser Pro Arg Glu Leu Arg Val Trp
965 970 975
Ala Pro Leu Phe Ser Gln Leu Gly Leu Arg Phe Leu Gln Glu Leu Ser
980 985 990
Glu Pro Gln Leu Arg Ala Met Leu Pro Val Leu Gln Gly Thr Ser Val
995 1000 1005
Thr Pro Ala Gln Ala Val Leu Leu Leu Gly Arg Leu Leu Pro Arg
1010 1015 1020
His Asp Leu Ser Leu Glu Glu Leu Cys Ser Leu His Leu Leu Leu
1025 1030 1035
Pro Gly Leu Ser Pro Gln Thr Leu Gln Ala Ile Pro Arg Arg Val
1040 1045 1050
Leu Val Gly Ala Cys Ser Cys Leu Ala Pro Glu Leu Ser Arg Leu
1055 1060 1065
Ser Ala Cys Gln Thr Ala Ala Leu Leu Gln Thr Phe Arg Val Lys
1070 1075 1080
Asp Gly Val Lys Asn Met Gly Thr Thr Gly Ala Gly Pro Ala Val
1085 1090 1095
Cys Ile Pro Gly Gln Pro Ile Pro Thr Thr Trp Pro Asp Cys Leu
1100 1105 1110
Leu Pro Leu Leu Pro Leu Lys Leu Leu Gln Leu Asp Ser Leu Ala
1115 1120 1125
Leu Leu Ala Asn Arg Arg Arg Tyr Trp Glu Leu Pro Trp Ser Glu
1130 1135 1140
Gln Gln Ala Gln Phe Leu Trp Lys Lys Met Gln Val Pro Thr Asn
1145 1150 1155
Leu Thr Leu Arg Asn Leu Gln Ala Leu Gly Thr Leu Ala Gly Gly
1160 1165 1170
Met Ser Cys Glu Phe Leu Gln Gln Ile Asn Ser Met Val Asp Phe
1175 1180 1185
Leu Glu Val Val His Met Ile Tyr Gln Leu Pro Thr Arg Val Arg
1190 1195 1200
Gly Ser Leu Arg Ala Cys Ile Trp Ala Glu Leu Gln Arg Arg Met
1205 1210 1215
Ala Met Pro Glu Pro Glu Trp Thr Thr Val Gly Pro Glu Leu Asn
1220 1225 1230
Gly Leu Asp Ser Lys Leu Leu Leu Asp Leu Pro Ile Gln Leu Met
1235 1240 1245
Asp Arg Leu Ser Asn Glu Ser Ile Met Leu Val Val Glu Leu Val
1250 1255 1260
Gln Arg Ala Pro Glu Gln Leu Leu Ala Leu Thr Pro Leu His Gln
1265 1270 1275
Ala Ala Leu Ala Glu Arg Ala Leu Gln Asn Leu Ala Pro Lys Glu
1280 1285 1290
Thr Pro Val Ser Gly Glu Val Leu Glu Thr Leu Gly Pro Leu Val
1295 1300 1305
Gly Phe Leu Gly Thr Glu Ser Thr Arg Gln Ile Pro Leu Gln Ile
1310 1315 1320
Leu Leu Ser His Leu Ser Gln Leu Gln Gly Phe Cys Leu Gly Glu
1325 1330 1335
Thr Phe Ala Thr Glu Leu Gly Trp Leu Leu Leu Gln Glu Ser Val
1340 1345 1350
Leu Gly Lys Pro Glu Leu Trp Ser Gln Asp Glu Val Glu Gln Ala
1355 1360 1365
Gly Arg Leu Val Phe Thr Leu Ser Thr Glu Ala Ile Ser Leu Ile
1370 1375 1380
Pro Arg Glu Ala Leu Gly Pro Glu Thr Leu Glu Arg Leu Leu Glu
1385 1390 1395
Lys Gln Gln Ser Trp Glu Gln Ser Arg Val Gly Gln Leu Cys Arg
1400 1405 1410
Glu Pro Gln Leu Ala Ala Lys Lys Ala Ala Leu Val Ala Gly Val
1415 1420 1425
Val Arg Pro Ala Ala Glu Asp Leu Pro Glu Pro Val Pro Asn Cys
1430 1435 1440
Ala Asp Val Arg Gly Thr Phe Pro Ala Ala Trp Ser Ala Thr Gln
1445 1450 1455
Ile Ala Glu Met Glu Leu Ser Asp Phe Glu Asp Cys Leu Thr Leu
1460 1465 1470
Phe Ala Gly Asp Pro Gly Leu Gly Pro Glu Glu Leu Arg Ala Ala
1475 1480 1485
Met Gly Lys Ala Lys Gln Leu Trp Gly Pro Pro Arg Gly Phe Arg
1490 1495 1500
Pro Glu Gln Ile Leu Gln Leu Gly Arg Leu Leu Ile Gly Leu Gly
1505 1510 1515
Asp Arg Glu Leu Gln Glu Leu Ile Leu Val Asp Trp Gly Val Leu
1520 1525 1530
Ser Thr Leu Gly Gln Ile Asp Gly Trp Ser Thr Thr Gln Leu Arg
1535 1540 1545
Ile Val Val Ser Ser Phe Leu Arg Gln Ser Gly Arg His Val Ser
1550 1555 1560
His Leu Asp Phe Val His Leu Thr Ala Leu Gly Tyr Thr Leu Cys
1565 1570 1575
Gly Leu Arg Pro Glu Glu Leu Gln His Ile Ser Ser Trp Glu Phe
1580 1585 1590
Ser Gln Ala Ala Leu Phe Leu Gly Thr Leu His Leu Gln Cys Ser
1595 1600 1605
Glu Glu Gln Leu Glu Val Leu Ala His Leu Leu Val Leu Pro Gly
1610 1615 1620
Gly Phe Gly Pro Ile Ser Asn Trp Gly Pro Glu Ile Phe Thr Glu
1625 1630 1635
Ile Gly Thr Ile Ala Ala Gly Ile Pro Asp Leu Ala Leu Ser Ala
1640 1645 1650
Leu Leu Arg Gly Gln Ile Gln Gly Val Thr Pro Leu Ala Ile Ser
1655 1660 1665
Val Ile Pro Pro Pro Lys Phe Ala Val Val Phe Ser Pro Ile Gln
1670 1675 1680
Leu Ser Ser Leu Thr Ser Ala Gln Ala Val Ala Val Thr Pro Glu
1685 1690 1695
Gln Met Ala Phe Leu Ser Pro Glu Gln Arg Arg Ala Val Ala Trp
1700 1705 1710
Ala Gln His Glu Gly Lys Glu Ser Pro Glu Gln Gln Gly Arg Ser
1715 1720 1725
Thr Ala Trp Gly Leu Gln Asp Trp Ser Arg Pro Ser Trp Ser Leu
1730 1735 1740
Val Leu Thr Ile Ser Phe Leu Gly His Leu Leu
1745 1750
<210> 3
<211> 5361
<212> DNA
<213> Mus musculus
<400> 3
gcccctactg ggcctcagtc tttggatgct ggtctctccc ttctgaagtc attcgtagcc 60
actctggacc aagctcctca gcgttccctc agccagtcac ggttctctgc gttcctggcc 120
aacatttctt catccttcca gcttgggagg atgggggagg gaccggtggg agagccccca 180
cctctccagc cccctgcact tcgacttcat gatttcctcg tgacactgag aggtagccca 240
gactgggagc caatgctagg gcttctggga gatgtgctgg cactcctggg acaggaacag 300
actccccggg actttttggt gcaccaggca ggtgtactgg gtggacttgt agaggcattg 360
ttgggagcgt tagttcctgg aggcccccct gcccccactc gacccccatg cacccgtgat 420
ggcccttctg actgtgtcct ggctgctgat tggttgcctt ctctgatgtt gttattagag 480
ggtacacgct ggcaggccct ggtgcagttg cagcccagtg tggacccaac caatgccaca 540
ggtcttgatg gtagagagcc agctcctcac tttttacagg gtctgctggg cttgcttacc 600
ccagcaggag agttgggctc tgaggaggct ctttggggtg gtctgctgcg cacagtgggg 660
gcccccctct atgctgcctt ccaggagggg ctactgcgag tcactcattc tctgcaagat 720
gaggtctttt ctattatggg acagccagag cctgatgcca gtgggcagtg ccagggaggc 780
aaccttcaac agctgctttt atggggcatg cggaacaacc tttcttggga cgcccgagca 840
ctgggttttc tatctggatc accacctcca ccccctgctc tcctgcactg cctgagcaga 900
ggtgtgcctc tgcccagggc ttcccagcct gcggctcaca tcagccctcg acagcggcga 960
gccatctctg tggaggccct ctgcgagaac cactcaggcc cagagccacc ctacagcatc 1020
tccaacttct ccatctactt gctctgccag cacatcaagc ctgccacccc gcggccccct 1080
cctaccaccc cacggcctcc tcctaccacc ccacagcccc ctcctaccac tacacagccc 1140
attcctgaca ctacacagcc ccctcctgtc accccaaggc ctcctcctac caccccacaa 1200
ccccctccta gcacagctgt catctgccag acagctgtat ggtacgcagt ctcgtgggca 1260
ccaggtgccc gaggttggct ccaagcctgc catgatcagt ttcctgatca atttctggat 1320
atgatctgcg gcaacctctc attttcagcc ctgtctggcc ccagtcgtcc tttggtaaag 1380
cagctctgtg ctggcttgct cccacccccc actagctgtc caccaggcct gatccctgtg 1440
cccctcaccc cagaaatatt ctggggctgt ttcctggaga atgagacact gtgggctgaa 1500
cggttgtgtg tggaggacag tctgcaggct gtgcccccga ggaaccaggc ttgggttcag 1560
catgtgtgtc ggggccccac cttggacgcc actgattttc caccgtgccg cgttggaccc 1620
tgtggggaac gctgcccaga tgggggcagc ttcctgctca tggtctgtgc caatgacact 1680
ctgtatgaag ccttggttcc cttctgggct tggctagcag gccaatgcag aattagtcgt 1740
ggaggaaatg atacttgctt tctagaaggc atgctgggcc ccttgttgcc ctctctgccc 1800
cctctgggac catccccact ctgtctggct cctggtcctt ttctgcttgg catgttatcc 1860
cagttgccac gctgtcagtc ctccgtgcca gccctcgccc accccacgcg cctacattac 1920
ctcctgcgcc tactgacctt ccttctgggt ccagggactg ggggtgccga gacgcagggg 1980
atgttaggtc aagccctgct gctctctagt ctcccagaca actgttcatt ctgggatgcc 2040
ttccgcccag agggccggag aagtgtactg aggacagtcg gagagtactt gcagcgggaa 2100
gagccaaccc caccaggctt agactcctcc ctcagcctcg gctctggtat gagcaagatg 2160
gagcttctgt cctgcttcag tcctgtactg tgggatctac tccagagaga gaagagcgtt 2220
tgggccctga ggaccctggt gaaggcctac ctgcgcatgc ctccagaaga ccttcagcag 2280
cttgtgcttt cagcagagat ggaggctgca cagggcttcc tgacgctcat gcttcgttcc 2340
tgggctaagc tgaaggttca accatccgag gagcaggcca tgggccgcct gacagccttg 2400
ctgctccagc ggtacccacg cctcacctcc caactcttta tcgacatgtc accgctcatc 2460
cccttcctgg ctgtccctga cctcatgcgc ttcccaccgt cccttttggc caacgacagt 2520
gtcctggctg ccatcaggga tcacagctca ggaatgaagc ctgaacagaa ggaggccctg 2580
gcaaaacgac tgctggcccc tgagctgttt ggagaagtgc ctgattggcc ccaggagctg 2640
ctgtgggcag ccctgcctct gcttccccat ctgcctctgg agagctttct ccagctcagc 2700
cctcaccaga tccaggccct ggaggatagc tggccagtag cagatcttgg gccgggacac 2760
gcccgacatg tgcttcgtag cctagtaaac cagagcatgg aggatgggga ggagcaggtg 2820
ctcaggcttg ggtccctcgc ctgtttcctg agtcctgagg agctacagag tctggtgccc 2880
ttgagtgatc caatggggcc tgtagaacag ggtctgctgg aatgtgcggc caatgggacc 2940
ctcagcccag aaggacgggt ggcatatgaa cttctgggag tgttgcgttc atctggagga 3000
actgtcttaa gcccccgaga gctgagggtc tgggcacctc tctttcccca gctgggcctc 3060
cgcttcctgc aggagctctc agagacccag cttagagcca tgcttcctgc cctacaggga 3120
gccagtgtca cacctgccca ggctgttctg ttgtttggaa ggctccttcc taagcatgat 3180
ctgtccctgg aggaactctg ctccctgcac cctctcctgc caggtctcag cccccagaca 3240
ctccaggcca tccctaagag agttctggtt ggtgcttgtt cctgcctggg ccctgaactg 3300
tcaaggcttt cagcttgcca gattgcagct ctgctgcaga cctttcgggt aaaagatggt 3360
gttaaaaata tgggtgcagc aggtgccggc tcagccgtgt gcattcctgg gcagcccacc 3420
acttggccag actgcctgct tcccctgctc ccattaaagc tgctacagct ggacgctgca 3480
gctcttctgg caaaccgaag actctatcgg cagctgcctt ggtctgagca acaggcacag 3540
tttctctgga agaaaatgca agtgcctacc aacctgagcc tgaggaatct gcaggctctg 3600
ggcaacttgg caggaggcat gacctgcgag tttctgcagc agatcagctc aatggttgac 3660
tttcttgatg tggtacacat gctctaccag ctgcccactg gtgttcgaga gagcctgcgg 3720
gcctgtatct ggacagagct acagcggagg atgacaatgc cagagccaga gctgaccacc 3780
ctagggccag aactgagtga acttgacaca aagctactcc tggacttgcc gatccagctg 3840
atggacagat tgtccaatga ttccattatg ttggtggtgg agatggtcca aggcgctcca 3900
gagcagctgc tggcactgac cccactccac cagacagcct tggcagagcg agcacttaaa 3960
aacctggctc caaaggagac cccaatctcc aaagaagtgc tggagacact gggccccttg 4020
gttggattcc tgggaataga gagcacgcga cggatccctt tacccattct actgtctcat 4080
ctcagtcagc tgcagggctt ctgcctagga gagacatttg ccacagagct gggatggctg 4140
ctgttgcagg agcctgttct tggaaaacca gaattgtgga gccaggatga aatagagcaa 4200
gctggacgcc tagtattcac tctgtctgct gaggctattt cctcgatccc cagggaggct 4260
ttgggcccag agacactgga gaggcttctg ggaaagcatc aaagctggga gcagagcaga 4320
gtgggccatc tgtgtgggga gtcacagctt gcccacaaga aagcagctct ggtagctggg 4380
attgtgcatc cagctgctga gggtctccaa gagcctgtac caaactgtgc agacatacgg 4440
ggaaccttcc cagcggcctg gtctgcgaca caaatctcag agatggaact ctcagacttt 4500
gaagactgcc tgtcactatt tgctggagat ccaggacttg gtcctgagga actacgggca 4560
gccatgggca aggccaagca gttgtggggt ccccctcgag gattccgtcc tgagcagatc 4620
ttgcagctgg gccgtctcct gataggtcta ggagaacggg aactgcagga gcttaccttg 4680
gtggactggg gtgtgctgag cagcctgggg caaatagatg gctggagttc catgcagctc 4740
cgagccgtgg tctccagttt cctaaggcag agtggtcggc atgtgagcca cctggacttc 4800
atttatctga cagcactggg ttacacagtc tgtggattgc gaccagagga gttacagcac 4860
atcagcagtt gggagtttag ccaagcagct ctcttcctgg gtagcttgca tctcccgtgc 4920
tctgaggaac agctggaagt tctggcctat ctccttgtgt tgcctggtgg ctttggccca 4980
gtcagtaact gggggcctga gatcttcact gaaattggca caatagcagc tggcatccca 5040
gacctggctc tttcagcatt actgcgggga cagatccaag gcctgactcc tcttgccatt 5100
tctgtcattc ctgctcccaa gtttgcagtg gtcttcaacc ccatccagtt atctagtctc 5160
accaggggtc aggccgtagc tgttactcct gaacagctgg cctatctgag tcctgagcag 5220
cggcgagcag ttgcatgggc ccaacacgaa gggaaggaga tcccagagca gctgggtcga 5280
aactcagcct ggggtctcta cgactggttc caagcctcct gggccctggc attgcccgtc 5340
agcatttttg gccacctatt a 5361
<210> 4
<211> 1787
<212> PRT
<213> Mus musculus
<400> 4
Ala Pro Thr Gly Pro Gln Ser Leu Asp Ala Gly Leu Ser Leu Leu Lys
1 5 10 15
Ser Phe Val Ala Thr Leu Asp Gln Ala Pro Gln Arg Ser Leu Ser Gln
20 25 30
Ser Arg Phe Ser Ala Phe Leu Ala Asn Ile Ser Ser Ser Phe Gln Leu
35 40 45
Gly Arg Met Gly Glu Gly Pro Val Gly Glu Pro Pro Pro Leu Gln Pro
50 55 60
Pro Ala Leu Arg Leu His Asp Phe Leu Val Thr Leu Arg Gly Ser Pro
65 70 75 80
Asp Trp Glu Pro Met Leu Gly Leu Leu Gly Asp Val Leu Ala Leu Leu
85 90 95
Gly Gln Glu Gln Thr Pro Arg Asp Phe Leu Val His Gln Ala Gly Val
100 105 110
Leu Gly Gly Leu Val Glu Ala Leu Leu Gly Ala Leu Val Pro Gly Gly
115 120 125
Pro Pro Ala Pro Thr Arg Pro Pro Cys Thr Arg Asp Gly Pro Ser Asp
130 135 140
Cys Val Leu Ala Ala Asp Trp Leu Pro Ser Leu Met Leu Leu Leu Glu
145 150 155 160
Gly Thr Arg Trp Gln Ala Leu Val Gln Leu Gln Pro Ser Val Asp Pro
165 170 175
Thr Asn Ala Thr Gly Leu Asp Gly Arg Glu Pro Ala Pro His Phe Leu
180 185 190
Gln Gly Leu Leu Gly Leu Leu Thr Pro Ala Gly Glu Leu Gly Ser Glu
195 200 205
Glu Ala Leu Trp Gly Gly Leu Leu Arg Thr Val Gly Ala Pro Leu Tyr
210 215 220
Ala Ala Phe Gln Glu Gly Leu Leu Arg Val Thr His Ser Leu Gln Asp
225 230 235 240
Glu Val Phe Ser Ile Met Gly Gln Pro Glu Pro Asp Ala Ser Gly Gln
245 250 255
Cys Gln Gly Gly Asn Leu Gln Gln Leu Leu Leu Trp Gly Met Arg Asn
260 265 270
Asn Leu Ser Trp Asp Ala Arg Ala Leu Gly Phe Leu Ser Gly Ser Pro
275 280 285
Pro Pro Pro Pro Ala Leu Leu His Cys Leu Ser Arg Gly Val Pro Leu
290 295 300
Pro Arg Ala Ser Gln Pro Ala Ala His Ile Ser Pro Arg Gln Arg Arg
305 310 315 320
Ala Ile Ser Val Glu Ala Leu Cys Glu Asn His Ser Gly Pro Glu Pro
325 330 335
Pro Tyr Ser Ile Ser Asn Phe Ser Ile Tyr Leu Leu Cys Gln His Ile
340 345 350
Lys Pro Ala Thr Pro Arg Pro Pro Pro Thr Thr Pro Arg Pro Pro Pro
355 360 365
Thr Thr Pro Gln Pro Pro Pro Thr Thr Thr Gln Pro Ile Pro Asp Thr
370 375 380
Thr Gln Pro Pro Pro Val Thr Pro Arg Pro Pro Pro Thr Thr Pro Gln
385 390 395 400
Pro Pro Pro Ser Thr Ala Val Ile Cys Gln Thr Ala Val Trp Tyr Ala
405 410 415
Val Ser Trp Ala Pro Gly Ala Arg Gly Trp Leu Gln Ala Cys His Asp
420 425 430
Gln Phe Pro Asp Gln Phe Leu Asp Met Ile Cys Gly Asn Leu Ser Phe
435 440 445
Ser Ala Leu Ser Gly Pro Ser Arg Pro Leu Val Lys Gln Leu Cys Ala
450 455 460
Gly Leu Leu Pro Pro Pro Thr Ser Cys Pro Pro Gly Leu Ile Pro Val
465 470 475 480
Pro Leu Thr Pro Glu Ile Phe Trp Gly Cys Phe Leu Glu Asn Glu Thr
485 490 495
Leu Trp Ala Glu Arg Leu Cys Val Glu Asp Ser Leu Gln Ala Val Pro
500 505 510
Pro Arg Asn Gln Ala Trp Val Gln His Val Cys Arg Gly Pro Thr Leu
515 520 525
Asp Ala Thr Asp Phe Pro Pro Cys Arg Val Gly Pro Cys Gly Glu Arg
530 535 540
Cys Pro Asp Gly Gly Ser Phe Leu Leu Met Val Cys Ala Asn Asp Thr
545 550 555 560
Leu Tyr Glu Ala Leu Val Pro Phe Trp Ala Trp Leu Ala Gly Gln Cys
565 570 575
Arg Ile Ser Arg Gly Gly Asn Asp Thr Cys Phe Leu Glu Gly Met Leu
580 585 590
Gly Pro Leu Leu Pro Ser Leu Pro Pro Leu Gly Pro Ser Pro Leu Cys
595 600 605
Leu Ala Pro Gly Pro Phe Leu Leu Gly Met Leu Ser Gln Leu Pro Arg
610 615 620
Cys Gln Ser Ser Val Pro Ala Leu Ala His Pro Thr Arg Leu His Tyr
625 630 635 640
Leu Leu Arg Leu Leu Thr Phe Leu Leu Gly Pro Gly Thr Gly Gly Ala
645 650 655
Glu Thr Gln Gly Met Leu Gly Gln Ala Leu Leu Leu Ser Ser Leu Pro
660 665 670
Asp Asn Cys Ser Phe Trp Asp Ala Phe Arg Pro Glu Gly Arg Arg Ser
675 680 685
Val Leu Arg Thr Val Gly Glu Tyr Leu Gln Arg Glu Glu Pro Thr Pro
690 695 700
Pro Gly Leu Asp Ser Ser Leu Ser Leu Gly Ser Gly Met Ser Lys Met
705 710 715 720
Glu Leu Leu Ser Cys Phe Ser Pro Val Leu Trp Asp Leu Leu Gln Arg
725 730 735
Glu Lys Ser Val Trp Ala Leu Arg Thr Leu Val Lys Ala Tyr Leu Arg
740 745 750
Met Pro Pro Glu Asp Leu Gln Gln Leu Val Leu Ser Ala Glu Met Glu
755 760 765
Ala Ala Gln Gly Phe Leu Thr Leu Met Leu Arg Ser Trp Ala Lys Leu
770 775 780
Lys Val Gln Pro Ser Glu Glu Gln Ala Met Gly Arg Leu Thr Ala Leu
785 790 795 800
Leu Leu Gln Arg Tyr Pro Arg Leu Thr Ser Gln Leu Phe Ile Asp Met
805 810 815
Ser Pro Leu Ile Pro Phe Leu Ala Val Pro Asp Leu Met Arg Phe Pro
820 825 830
Pro Ser Leu Leu Ala Asn Asp Ser Val Leu Ala Ala Ile Arg Asp His
835 840 845
Ser Ser Gly Met Lys Pro Glu Gln Lys Glu Ala Leu Ala Lys Arg Leu
850 855 860
Leu Ala Pro Glu Leu Phe Gly Glu Val Pro Asp Trp Pro Gln Glu Leu
865 870 875 880
Leu Trp Ala Ala Leu Pro Leu Leu Pro His Leu Pro Leu Glu Ser Phe
885 890 895
Leu Gln Leu Ser Pro His Gln Ile Gln Ala Leu Glu Asp Ser Trp Pro
900 905 910
Val Ala Asp Leu Gly Pro Gly His Ala Arg His Val Leu Arg Ser Leu
915 920 925
Val Asn Gln Ser Met Glu Asp Gly Glu Glu Gln Val Leu Arg Leu Gly
930 935 940
Ser Leu Ala Cys Phe Leu Ser Pro Glu Glu Leu Gln Ser Leu Val Pro
945 950 955 960
Leu Ser Asp Pro Met Gly Pro Val Glu Gln Gly Leu Leu Glu Cys Ala
965 970 975
Ala Asn Gly Thr Leu Ser Pro Glu Gly Arg Val Ala Tyr Glu Leu Leu
980 985 990
Gly Val Leu Arg Ser Ser Gly Gly Thr Val Leu Ser Pro Arg Glu Leu
995 1000 1005
Arg Val Trp Ala Pro Leu Phe Pro Gln Leu Gly Leu Arg Phe Leu
1010 1015 1020
Gln Glu Leu Ser Glu Thr Gln Leu Arg Ala Met Leu Pro Ala Leu
1025 1030 1035
Gln Gly Ala Ser Val Thr Pro Ala Gln Ala Val Leu Leu Phe Gly
1040 1045 1050
Arg Leu Leu Pro Lys His Asp Leu Ser Leu Glu Glu Leu Cys Ser
1055 1060 1065
Leu His Pro Leu Leu Pro Gly Leu Ser Pro Gln Thr Leu Gln Ala
1070 1075 1080
Ile Pro Lys Arg Val Leu Val Gly Ala Cys Ser Cys Leu Gly Pro
1085 1090 1095
Glu Leu Ser Arg Leu Ser Ala Cys Gln Ile Ala Ala Leu Leu Gln
1100 1105 1110
Thr Phe Arg Val Lys Asp Gly Val Lys Asn Met Gly Ala Ala Gly
1115 1120 1125
Ala Gly Ser Ala Val Cys Ile Pro Gly Gln Pro Thr Thr Trp Pro
1130 1135 1140
Asp Cys Leu Leu Pro Leu Leu Pro Leu Lys Leu Leu Gln Leu Asp
1145 1150 1155
Ala Ala Ala Leu Leu Ala Asn Arg Arg Leu Tyr Arg Gln Leu Pro
1160 1165 1170
Trp Ser Glu Gln Gln Ala Gln Phe Leu Trp Lys Lys Met Gln Val
1175 1180 1185
Pro Thr Asn Leu Ser Leu Arg Asn Leu Gln Ala Leu Gly Asn Leu
1190 1195 1200
Ala Gly Gly Met Thr Cys Glu Phe Leu Gln Gln Ile Ser Ser Met
1205 1210 1215
Val Asp Phe Leu Asp Val Val His Met Leu Tyr Gln Leu Pro Thr
1220 1225 1230
Gly Val Arg Glu Ser Leu Arg Ala Cys Ile Trp Thr Glu Leu Gln
1235 1240 1245
Arg Arg Met Thr Met Pro Glu Pro Glu Leu Thr Thr Leu Gly Pro
1250 1255 1260
Glu Leu Ser Glu Leu Asp Thr Lys Leu Leu Leu Asp Leu Pro Ile
1265 1270 1275
Gln Leu Met Asp Arg Leu Ser Asn Asp Ser Ile Met Leu Val Val
1280 1285 1290
Glu Met Val Gln Gly Ala Pro Glu Gln Leu Leu Ala Leu Thr Pro
1295 1300 1305
Leu His Gln Thr Ala Leu Ala Glu Arg Ala Leu Lys Asn Leu Ala
1310 1315 1320
Pro Lys Glu Thr Pro Ile Ser Lys Glu Val Leu Glu Thr Leu Gly
1325 1330 1335
Pro Leu Val Gly Phe Leu Gly Ile Glu Ser Thr Arg Arg Ile Pro
1340 1345 1350
Leu Pro Ile Leu Leu Ser His Leu Ser Gln Leu Gln Gly Phe Cys
1355 1360 1365
Leu Gly Glu Thr Phe Ala Thr Glu Leu Gly Trp Leu Leu Leu Gln
1370 1375 1380
Glu Pro Val Leu Gly Lys Pro Glu Leu Trp Ser Gln Asp Glu Ile
1385 1390 1395
Glu Gln Ala Gly Arg Leu Val Phe Thr Leu Ser Ala Glu Ala Ile
1400 1405 1410
Ser Ser Ile Pro Arg Glu Ala Leu Gly Pro Glu Thr Leu Glu Arg
1415 1420 1425
Leu Leu Gly Lys His Gln Ser Trp Glu Gln Ser Arg Val Gly His
1430 1435 1440
Leu Cys Gly Glu Ser Gln Leu Ala His Lys Lys Ala Ala Leu Val
1445 1450 1455
Ala Gly Ile Val His Pro Ala Ala Glu Gly Leu Gln Glu Pro Val
1460 1465 1470
Pro Asn Cys Ala Asp Ile Arg Gly Thr Phe Pro Ala Ala Trp Ser
1475 1480 1485
Ala Thr Gln Ile Ser Glu Met Glu Leu Ser Asp Phe Glu Asp Cys
1490 1495 1500
Leu Ser Leu Phe Ala Gly Asp Pro Gly Leu Gly Pro Glu Glu Leu
1505 1510 1515
Arg Ala Ala Met Gly Lys Ala Lys Gln Leu Trp Gly Pro Pro Arg
1520 1525 1530
Gly Phe Arg Pro Glu Gln Ile Leu Gln Leu Gly Arg Leu Leu Ile
1535 1540 1545
Gly Leu Gly Glu Arg Glu Leu Gln Glu Leu Thr Leu Val Asp Trp
1550 1555 1560
Gly Val Leu Ser Ser Leu Gly Gln Ile Asp Gly Trp Ser Ser Met
1565 1570 1575
Gln Leu Arg Ala Val Val Ser Ser Phe Leu Arg Gln Ser Gly Arg
1580 1585 1590
His Val Ser His Leu Asp Phe Ile Tyr Leu Thr Ala Leu Gly Tyr
1595 1600 1605
Thr Val Cys Gly Leu Arg Pro Glu Glu Leu Gln His Ile Ser Ser
1610 1615 1620
Trp Glu Phe Ser Gln Ala Ala Leu Phe Leu Gly Ser Leu His Leu
1625 1630 1635
Pro Cys Ser Glu Glu Gln Leu Glu Val Leu Ala Tyr Leu Leu Val
1640 1645 1650
Leu Pro Gly Gly Phe Gly Pro Val Ser Asn Trp Gly Pro Glu Ile
1655 1660 1665
Phe Thr Glu Ile Gly Thr Ile Ala Ala Gly Ile Pro Asp Leu Ala
1670 1675 1680
Leu Ser Ala Leu Leu Arg Gly Gln Ile Gln Gly Leu Thr Pro Leu
1685 1690 1695
Ala Ile Ser Val Ile Pro Ala Pro Lys Phe Ala Val Val Phe Asn
1700 1705 1710
Pro Ile Gln Leu Ser Ser Leu Thr Arg Gly Gln Ala Val Ala Val
1715 1720 1725
Thr Pro Glu Gln Leu Ala Tyr Leu Ser Pro Glu Gln Arg Arg Ala
1730 1735 1740
Val Ala Trp Ala Gln His Glu Gly Lys Glu Ile Pro Glu Gln Leu
1745 1750 1755
Gly Arg Asn Ser Ala Trp Gly Leu Tyr Asp Trp Phe Gln Ala Ser
1760 1765 1770
Trp Ala Leu Ala Leu Pro Val Ser Ile Phe Gly His Leu Leu
1775 1780 1785
<210> 5
<211> 2436
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 5
atggctctca gcctctggcc cctgctgctg ctgctgctgc tgctgctgct gctgtccttt 60
gcagtgactc tggcccctac tgggcctcat tccctggacc ctggtctctc cttcctgaag 120
tcattgctct ccactctgga ccaggctccc cagggctccc tgagccgctc acggttcttt 180
acattcctgg ccaacatttc ttcttccttt gagcctggga gaatggggga aggaccagta 240
ggagagcccc cacctctcca gccgcctgct ctgcggctcc atgattttct agtgacactg 300
agaggtagcc ccgactggga gccaatgcta gggctgctag gggatatgct ggcactgctg 360
ggacaggagc agactccccg agatttcctg gtgcaccagg caggggtgct gggtggactt 420
gtggaggtgc tgctgggagc cttagttcct gggggccccc ctaccccaac tcggccccca 480
tgcacccgtg atgggccgtc tgactgtgtc ctggctgctg actggttgcc ttctctgctg 540
ctgttgttag agggcacacg ctggcaagct ctggtgcagg tgcagcccag tgtggacccc 600
accaatgcca caggcctcga tgggagggag gcagctcctc actttttgca gggtctgttg 660
ggtttgctta ccccaacagg ggagctaggc tccaaggagg ctctttgggg cggtctgcta 720
cgcacagtgg gggcccccct ctatgctgcc tttcaggagg ggctgctccg tgtcactcac 780
tccctgcagg atgaggtctt ctccattttg gggcagccag agcctgatac caatgggcag 840
tgccagggag gtaaccttca acagctgctc ttatggggcg tccggcacaa cctttcctgg 900
gatgtccagg cgctgggctt tctgtctgga tcaccacccc caccccctgc cctccttcac 960
tgcctgagca cgggcgtgcc tctgcccaga gcttctcagc cgtcagccca catcagccca 1020
cgccaacggc gagccatcac tgtggaggcc ctctgtgaga accacttagg cccagcacca 1080
ccctacagca tttccaactt ctccatccac ttgctctgcc agcacaccaa gcctgccact 1140
ccacagcccc atcccagcac cactgccatc tgccagacag ctgtgtggta tgcagtgtcc 1200
tgggcaccag gtgcccaagg ctggctacag gcctgccacg accagtttcc tgatgagttt 1260
ttggatgcga tctgcagtaa cctctccttt tcagccctgt ctggctccaa ccgccgcctg 1320
gtgaagcggc tctgtgctgg cctgctccca ccccctacca gctgccctga aggcctgccc 1380
cctgttcccc tcaccccaga catcttttgg ggctgcttct tggagaatga gactctgtgg 1440
gctgagcgac tgtgtgggga ggcaagtcta caggctgtgc cccccagcaa ccaggcttgg 1500
gtccagcatg tgtgccaggg ccccacccca gatgtcactg cctccccacc atgccacatt 1560
ggaccctgtg gggaacgctg cccggatggg ggcagcttcc tggtgatggt ctgtgccaat 1620
gacaccatgt atgaggtcct ggtgcccttc tggccttggc tagcaggcca atgcaggata 1680
agtcgtgggg gcaatgacac ttgcttccta gaagggctgc tgggccccct tctgccctct 1740
ctgccaccac tgggaccatc cccactctgt ctgacccctg gccccttcct ccttggcatg 1800
ctatcccagt tgccacgctg tcagtcctct gtcccagctc ttgctcaccc cacacgccta 1860
cactatctcc tccgcctgct gaccttcctc ttgggtccag gggctggggg cgctgaggcc 1920
caggggatgc tgggtcgggc cctactgctc tccagtctcc cagacaactg ctccttctgg 1980
gatgcctttc gcccagaggg ccggcgcagt gtgctacgga cgattgggga atacctggaa 2040
caagatgagg agcagccaac cccatcaggc tttgaaccca ctgtcaaccc cagctctggt 2100
ataagcaaga tggagctgct ggcctgcctg tcatacgaaa ccgagatact gacagtagaa 2160
tatggccttc tgccaatcgg gaagattgtg gagaaacgga tagaatgcac agtttactct 2220
gtcgataaca atggtaacat ttatactcag ccagttgccc agtggcacga ccggggagag 2280
caggaagtat tcgaatactg tctggaggat ggaagtctca ttagggccac taaggaccac 2340
aaatttatga cagtcgatgg ccagatgctg cctatagacg aaatctttga gcgagagttg 2400
gacctcatgc gagttgacaa ccttcctaat taatag 2436
<210> 6
<211> 810
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 6
Met Ala Leu Ser Leu Trp Pro Leu Leu Leu Leu Leu Leu Leu Leu Leu
1 5 10 15
Leu Leu Ser Phe Ala Val Thr Leu Ala Pro Thr Gly Pro His Ser Leu
20 25 30
Asp Pro Gly Leu Ser Phe Leu Lys Ser Leu Leu Ser Thr Leu Asp Gln
35 40 45
Ala Pro Gln Gly Ser Leu Ser Arg Ser Arg Phe Phe Thr Phe Leu Ala
50 55 60
Asn Ile Ser Ser Ser Phe Glu Pro Gly Arg Met Gly Glu Gly Pro Val
65 70 75 80
Gly Glu Pro Pro Pro Leu Gln Pro Pro Ala Leu Arg Leu His Asp Phe
85 90 95
Leu Val Thr Leu Arg Gly Ser Pro Asp Trp Glu Pro Met Leu Gly Leu
100 105 110
Leu Gly Asp Met Leu Ala Leu Leu Gly Gln Glu Gln Thr Pro Arg Asp
115 120 125
Phe Leu Val His Gln Ala Gly Val Leu Gly Gly Leu Val Glu Val Leu
130 135 140
Leu Gly Ala Leu Val Pro Gly Gly Pro Pro Thr Pro Thr Arg Pro Pro
145 150 155 160
Cys Thr Arg Asp Gly Pro Ser Asp Cys Val Leu Ala Ala Asp Trp Leu
165 170 175
Pro Ser Leu Leu Leu Leu Leu Glu Gly Thr Arg Trp Gln Ala Leu Val
180 185 190
Gln Val Gln Pro Ser Val Asp Pro Thr Asn Ala Thr Gly Leu Asp Gly
195 200 205
Arg Glu Ala Ala Pro His Phe Leu Gln Gly Leu Leu Gly Leu Leu Thr
210 215 220
Pro Thr Gly Glu Leu Gly Ser Lys Glu Ala Leu Trp Gly Gly Leu Leu
225 230 235 240
Arg Thr Val Gly Ala Pro Leu Tyr Ala Ala Phe Gln Glu Gly Leu Leu
245 250 255
Arg Val Thr His Ser Leu Gln Asp Glu Val Phe Ser Ile Leu Gly Gln
260 265 270
Pro Glu Pro Asp Thr Asn Gly Gln Cys Gln Gly Gly Asn Leu Gln Gln
275 280 285
Leu Leu Leu Trp Gly Val Arg His Asn Leu Ser Trp Asp Val Gln Ala
290 295 300
Leu Gly Phe Leu Ser Gly Ser Pro Pro Pro Pro Pro Ala Leu Leu His
305 310 315 320
Cys Leu Ser Thr Gly Val Pro Leu Pro Arg Ala Ser Gln Pro Ser Ala
325 330 335
His Ile Ser Pro Arg Gln Arg Arg Ala Ile Thr Val Glu Ala Leu Cys
340 345 350
Glu Asn His Leu Gly Pro Ala Pro Pro Tyr Ser Ile Ser Asn Phe Ser
355 360 365
Ile His Leu Leu Cys Gln His Thr Lys Pro Ala Thr Pro Gln Pro His
370 375 380
Pro Ser Thr Thr Ala Ile Cys Gln Thr Ala Val Trp Tyr Ala Val Ser
385 390 395 400
Trp Ala Pro Gly Ala Gln Gly Trp Leu Gln Ala Cys His Asp Gln Phe
405 410 415
Pro Asp Glu Phe Leu Asp Ala Ile Cys Ser Asn Leu Ser Phe Ser Ala
420 425 430
Leu Ser Gly Ser Asn Arg Arg Leu Val Lys Arg Leu Cys Ala Gly Leu
435 440 445
Leu Pro Pro Pro Thr Ser Cys Pro Glu Gly Leu Pro Pro Val Pro Leu
450 455 460
Thr Pro Asp Ile Phe Trp Gly Cys Phe Leu Glu Asn Glu Thr Leu Trp
465 470 475 480
Ala Glu Arg Leu Cys Gly Glu Ala Ser Leu Gln Ala Val Pro Pro Ser
485 490 495
Asn Gln Ala Trp Val Gln His Val Cys Gln Gly Pro Thr Pro Asp Val
500 505 510
Thr Ala Ser Pro Pro Cys His Ile Gly Pro Cys Gly Glu Arg Cys Pro
515 520 525
Asp Gly Gly Ser Phe Leu Val Met Val Cys Ala Asn Asp Thr Met Tyr
530 535 540
Glu Val Leu Val Pro Phe Trp Pro Trp Leu Ala Gly Gln Cys Arg Ile
545 550 555 560
Ser Arg Gly Gly Asn Asp Thr Cys Phe Leu Glu Gly Leu Leu Gly Pro
565 570 575
Leu Leu Pro Ser Leu Pro Pro Leu Gly Pro Ser Pro Leu Cys Leu Thr
580 585 590
Pro Gly Pro Phe Leu Leu Gly Met Leu Ser Gln Leu Pro Arg Cys Gln
595 600 605
Ser Ser Val Pro Ala Leu Ala His Pro Thr Arg Leu His Tyr Leu Leu
610 615 620
Arg Leu Leu Thr Phe Leu Leu Gly Pro Gly Ala Gly Gly Ala Glu Ala
625 630 635 640
Gln Gly Met Leu Gly Arg Ala Leu Leu Leu Ser Ser Leu Pro Asp Asn
645 650 655
Cys Ser Phe Trp Asp Ala Phe Arg Pro Glu Gly Arg Arg Ser Val Leu
660 665 670
Arg Thr Ile Gly Glu Tyr Leu Glu Gln Asp Glu Glu Gln Pro Thr Pro
675 680 685
Ser Gly Phe Glu Pro Thr Val Asn Pro Ser Ser Gly Ile Ser Lys Met
690 695 700
Glu Leu Leu Ala Cys Leu Ser Tyr Glu Thr Glu Ile Leu Thr Val Glu
705 710 715 720
Tyr Gly Leu Leu Pro Ile Gly Lys Ile Val Glu Lys Arg Ile Glu Cys
725 730 735
Thr Val Tyr Ser Val Asp Asn Asn Gly Asn Ile Tyr Thr Gln Pro Val
740 745 750
Ala Gln Trp His Asp Arg Gly Glu Gln Glu Val Phe Glu Tyr Cys Leu
755 760 765
Glu Asp Gly Ser Leu Ile Arg Ala Thr Lys Asp His Lys Phe Met Thr
770 775 780
Val Asp Gly Gln Met Leu Pro Ile Asp Glu Ile Phe Glu Arg Glu Leu
785 790 795 800
Asp Leu Met Arg Val Asp Asn Leu Pro Asn
805 810
<210> 7
<211> 2550
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 7
atggctctga gcctccagcc ccagctgctc cttctcctgt cgctcctgcc gcaggaagtg 60
acttcagccc ctactgggcc tcagtctttg gatgctggtc tctcccttct gaagtcattc 120
gtagccactc tggaccaagc tcctcagcgt tccctcagcc agtcacggtt ctctgcgttc 180
ctggccaaca tttcttcatc cttccagctt gggaggatgg gggagggacc ggtgggagag 240
cccccacctc tccagccccc tgcacttcga cttcatgatt tcctcgtgac actgagaggt 300
agcccagact gggagccaat gctagggctt ctgggagatg tgctggcact cctgggacag 360
gaacagactc cccgggactt tttggtgcac caggcaggtg tactgggtgg acttgtagag 420
gcattgttgg gagcgttagt tcctggaggc ccccctgccc ccactcgacc cccatgcacc 480
cgtgatggcc cttctgactg tgtcctggct gctgattggt tgccttctct gatgttgtta 540
ttagagggta cacgctggca ggccctggtg cagttgcagc ccagtgtgga cccaaccaat 600
gccacaggtc ttgatggtag agagccagct cctcactttt tacagggtct gctgggcttg 660
cttaccccag caggagagtt gggctctgag gaggctcttt ggggtggtct gctgcgcaca 720
gtgggggccc ccctctatgc tgccttccag gaggggctac tgcgagtcac tcattctctg 780
caagatgagg tcttttctat tatgggacag ccagagcctg atgccagtgg gcagtgccag 840
ggaggcaacc ttcaacagct gcttttatgg ggcatgcgga acaacctttc ttgggacgcc 900
cgagcactgg gttttctatc tggatcacca cctccacccc ctgctctcct gcactgcctg 960
agcagaggtg tgcctctgcc cagggcttcc cagcctgcgg ctcacatcag ccctcgacag 1020
cggcgagcca tctctgtgga ggccctctgc gagaaccact caggcccaga gccaccctac 1080
agcatctcca acttctccat ctacttgctc tgccagcaca tcaagcctgc caccccgcgg 1140
ccccctccta ccaccccacg gcctcctcct accaccccac agccccctcc taccactaca 1200
cagcccattc ctgacactac acagccccct cctgtcaccc caaggcctcc tcctaccacc 1260
ccacaacccc ctcctagcac agctgtcatc tgccagacag ctgtatggta cgcagtctcg 1320
tgggcaccag gtgcccgagg ttggctccaa gcctgccatg atcagtttcc tgatcaattt 1380
ctggatatga tctgcggcaa cctctcattt tcagccctgt ctggccccag tcgtcctttg 1440
gtaaagcagc tctgtgctgg cttgctccca ccccccacta gctgtccacc aggcctgatc 1500
cctgtgcccc tcaccccaga aatattctgg ggctgtttcc tggagaatga gacactgtgg 1560
gctgaacggt tgtgtgtgga ggacagtctg caggctgtgc ccccgaggaa ccaggcttgg 1620
gttcagcatg tgtgtcgggg ccccaccttg gacgccactg attttccacc gtgccgcgtt 1680
ggaccctgtg gggaacgctg cccagatggg ggcagcttcc tgctcatggt ctgtgccaat 1740
gacactctgt atgaagcctt ggttcccttc tgggcttggc tagcaggcca atgcagaatt 1800
agtcgtggag gaaatgatac ttgctttcta gaaggcatgc tgggcccctt gttgccctct 1860
ctgccccctc tgggaccatc cccactctgt ctggctcctg gtccttttct gcttggcatg 1920
ttatcccagt tgccacgctg tcagtcctcc gtgccagccc tcgcccaccc cacgcgccta 1980
cattacctcc tgcgcctact gaccttcctt ctgggtccag ggactggggg tgccgagacg 2040
caggggatgt taggtcaagc cctgctgctc tctagtctcc cagacaactg ttcattctgg 2100
gatgccttcc gcccagaggg ccggagaagt gtactgagga cagtcggaga gtacttgcag 2160
cgggaagagc caaccccacc aggcttagac tcctccctca gcctcggctc tggtatgagc 2220
aagatggagc ttctgtcctg cctgtcatac gaaaccgaga tactgacagt agaatatggc 2280
cttctgccaa tcgggaagat tgtggagaaa cggatagaat gcacagttta ctctgtcgat 2340
aacaatggta acatttatac tcagccagtt gcccagtggc acgaccgggg agagcaggaa 2400
gtattcgaat actgtctgga ggatggaagt ctcattaggg ccactaagga ccacaaattt 2460
atgacagtcg atggccagat gctgcctata gacgaaatct ttgagcgaga gttggacctc 2520
atgcgagttg acaaccttcc taattaatag 2550
<210> 8
<211> 848
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 8
Met Ala Leu Ser Leu Gln Pro Gln Leu Leu Leu Leu Leu Ser Leu Leu
1 5 10 15
Pro Gln Glu Val Thr Ser Ala Pro Thr Gly Pro Gln Ser Leu Asp Ala
20 25 30
Gly Leu Ser Leu Leu Lys Ser Phe Val Ala Thr Leu Asp Gln Ala Pro
35 40 45
Gln Arg Ser Leu Ser Gln Ser Arg Phe Ser Ala Phe Leu Ala Asn Ile
50 55 60
Ser Ser Ser Phe Gln Leu Gly Arg Met Gly Glu Gly Pro Val Gly Glu
65 70 75 80
Pro Pro Pro Leu Gln Pro Pro Ala Leu Arg Leu His Asp Phe Leu Val
85 90 95
Thr Leu Arg Gly Ser Pro Asp Trp Glu Pro Met Leu Gly Leu Leu Gly
100 105 110
Asp Val Leu Ala Leu Leu Gly Gln Glu Gln Thr Pro Arg Asp Phe Leu
115 120 125
Val His Gln Ala Gly Val Leu Gly Gly Leu Val Glu Ala Leu Leu Gly
130 135 140
Ala Leu Val Pro Gly Gly Pro Pro Ala Pro Thr Arg Pro Pro Cys Thr
145 150 155 160
Arg Asp Gly Pro Ser Asp Cys Val Leu Ala Ala Asp Trp Leu Pro Ser
165 170 175
Leu Met Leu Leu Leu Glu Gly Thr Arg Trp Gln Ala Leu Val Gln Leu
180 185 190
Gln Pro Ser Val Asp Pro Thr Asn Ala Thr Gly Leu Asp Gly Arg Glu
195 200 205
Pro Ala Pro His Phe Leu Gln Gly Leu Leu Gly Leu Leu Thr Pro Ala
210 215 220
Gly Glu Leu Gly Ser Glu Glu Ala Leu Trp Gly Gly Leu Leu Arg Thr
225 230 235 240
Val Gly Ala Pro Leu Tyr Ala Ala Phe Gln Glu Gly Leu Leu Arg Val
245 250 255
Thr His Ser Leu Gln Asp Glu Val Phe Ser Ile Met Gly Gln Pro Glu
260 265 270
Pro Asp Ala Ser Gly Gln Cys Gln Gly Gly Asn Leu Gln Gln Leu Leu
275 280 285
Leu Trp Gly Met Arg Asn Asn Leu Ser Trp Asp Ala Arg Ala Leu Gly
290 295 300
Phe Leu Ser Gly Ser Pro Pro Pro Pro Pro Ala Leu Leu His Cys Leu
305 310 315 320
Ser Arg Gly Val Pro Leu Pro Arg Ala Ser Gln Pro Ala Ala His Ile
325 330 335
Ser Pro Arg Gln Arg Arg Ala Ile Ser Val Glu Ala Leu Cys Glu Asn
340 345 350
His Ser Gly Pro Glu Pro Pro Tyr Ser Ile Ser Asn Phe Ser Ile Tyr
355 360 365
Leu Leu Cys Gln His Ile Lys Pro Ala Thr Pro Arg Pro Pro Pro Thr
370 375 380
Thr Pro Arg Pro Pro Pro Thr Thr Pro Gln Pro Pro Pro Thr Thr Thr
385 390 395 400
Gln Pro Ile Pro Asp Thr Thr Gln Pro Pro Pro Val Thr Pro Arg Pro
405 410 415
Pro Pro Thr Thr Pro Gln Pro Pro Pro Ser Thr Ala Val Ile Cys Gln
420 425 430
Thr Ala Val Trp Tyr Ala Val Ser Trp Ala Pro Gly Ala Arg Gly Trp
435 440 445
Leu Gln Ala Cys His Asp Gln Phe Pro Asp Gln Phe Leu Asp Met Ile
450 455 460
Cys Gly Asn Leu Ser Phe Ser Ala Leu Ser Gly Pro Ser Arg Pro Leu
465 470 475 480
Val Lys Gln Leu Cys Ala Gly Leu Leu Pro Pro Pro Thr Ser Cys Pro
485 490 495
Pro Gly Leu Ile Pro Val Pro Leu Thr Pro Glu Ile Phe Trp Gly Cys
500 505 510
Phe Leu Glu Asn Glu Thr Leu Trp Ala Glu Arg Leu Cys Val Glu Asp
515 520 525
Ser Leu Gln Ala Val Pro Pro Arg Asn Gln Ala Trp Val Gln His Val
530 535 540
Cys Arg Gly Pro Thr Leu Asp Ala Thr Asp Phe Pro Pro Cys Arg Val
545 550 555 560
Gly Pro Cys Gly Glu Arg Cys Pro Asp Gly Gly Ser Phe Leu Leu Met
565 570 575
Val Cys Ala Asn Asp Thr Leu Tyr Glu Ala Leu Val Pro Phe Trp Ala
580 585 590
Trp Leu Ala Gly Gln Cys Arg Ile Ser Arg Gly Gly Asn Asp Thr Cys
595 600 605
Phe Leu Glu Gly Met Leu Gly Pro Leu Leu Pro Ser Leu Pro Pro Leu
610 615 620
Gly Pro Ser Pro Leu Cys Leu Ala Pro Gly Pro Phe Leu Leu Gly Met
625 630 635 640
Leu Ser Gln Leu Pro Arg Cys Gln Ser Ser Val Pro Ala Leu Ala His
645 650 655
Pro Thr Arg Leu His Tyr Leu Leu Arg Leu Leu Thr Phe Leu Leu Gly
660 665 670
Pro Gly Thr Gly Gly Ala Glu Thr Gln Gly Met Leu Gly Gln Ala Leu
675 680 685
Leu Leu Ser Ser Leu Pro Asp Asn Cys Ser Phe Trp Asp Ala Phe Arg
690 695 700
Pro Glu Gly Arg Arg Ser Val Leu Arg Thr Val Gly Glu Tyr Leu Gln
705 710 715 720
Arg Glu Glu Pro Thr Pro Pro Gly Leu Asp Ser Ser Leu Ser Leu Gly
725 730 735
Ser Gly Met Ser Lys Met Glu Leu Leu Ser Cys Leu Ser Tyr Glu Thr
740 745 750
Glu Ile Leu Thr Val Glu Tyr Gly Leu Leu Pro Ile Gly Lys Ile Val
755 760 765
Glu Lys Arg Ile Glu Cys Thr Val Tyr Ser Val Asp Asn Asn Gly Asn
770 775 780
Ile Tyr Thr Gln Pro Val Ala Gln Trp His Asp Arg Gly Glu Gln Glu
785 790 795 800
Val Phe Glu Tyr Cys Leu Glu Asp Gly Ser Leu Ile Arg Ala Thr Lys
805 810 815
Asp His Lys Phe Met Thr Val Asp Gly Gln Met Leu Pro Ile Asp Glu
820 825 830
Ile Phe Glu Arg Glu Leu Asp Leu Met Arg Val Asp Asn Leu Pro Asn
835 840 845
<210> 9
<211> 60
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
oligonucleotide
<400> 9
gctctcagcc tctggcccct gctgctgctg ctgctgctgc tgctgctgct gtcctttgca 60
<210> 10
<211> 20
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 10
Ala Leu Ser Leu Trp Pro Leu Leu Leu Leu Leu Leu Leu Leu Leu Leu
1 5 10 15
Leu Ser Phe Ala
20
<210> 11
<211> 63
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
oligonucleotide
<400> 11
gctctgagcc tccagcccca gctgctcctt ctcctgtcgc tcctgccgca ggaagtgact 60
tca 63
<210> 12
<211> 21
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 12
Ala Leu Ser Leu Gln Pro Gln Leu Leu Leu Leu Leu Ser Leu Leu Pro
1 5 10 15
Gln Glu Val Thr Ser
20
<210> 13
<211> 306
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 13
tgcctgtcat acgaaaccga gatactgaca gtagaatatg gccttctgcc aatcgggaag 60
attgtggaga aacggataga atgcacagtt tactctgtcg ataacaatgg taacatttat 120
actcagccag ttgcccagtg gcacgaccgg ggagagcagg aagtattcga atactgtctg 180
gaggatggaa gtctcattag ggccactaag gaccacaaat ttatgacagt cgatggccag 240
atgctgccta tagacgaaat ctttgagcga gagttggacc tcatgcgagt tgacaacctt 300
cctaat 306
<210> 14
<211> 102
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 14
Cys Leu Ser Tyr Glu Thr Glu Ile Leu Thr Val Glu Tyr Gly Leu Leu
1 5 10 15
Pro Ile Gly Lys Ile Val Glu Lys Arg Ile Glu Cys Thr Val Tyr Ser
20 25 30
Val Asp Asn Asn Gly Asn Ile Tyr Thr Gln Pro Val Ala Gln Trp His
35 40 45
Asp Arg Gly Glu Gln Glu Val Phe Glu Tyr Cys Leu Glu Asp Gly Ser
50 55 60
Leu Ile Arg Ala Thr Lys Asp His Lys Phe Met Thr Val Asp Gly Gln
65 70 75 80
Met Leu Pro Ile Asp Glu Ile Phe Glu Arg Glu Leu Asp Leu Met Arg
85 90 95
Val Asp Asn Leu Pro Asn
100
<210> 15
<211> 687
<212> PRT
<213> Homo sapiens
<400> 15
Val Thr Leu Ala Pro Thr Gly Pro His Ser Leu Asp Pro Gly Leu Ser
1 5 10 15
Phe Leu Lys Ser Leu Leu Ser Thr Leu Asp Gln Ala Pro Gln Gly Ser
20 25 30
Leu Ser Arg Ser Arg Phe Phe Thr Phe Leu Ala Asn Ile Ser Ser Ser
35 40 45
Phe Glu Pro Gly Arg Met Gly Glu Gly Pro Val Gly Glu Pro Pro Pro
50 55 60
Leu Gln Pro Pro Ala Leu Arg Leu His Asp Phe Leu Val Thr Leu Arg
65 70 75 80
Gly Ser Pro Asp Trp Glu Pro Met Leu Gly Leu Leu Gly Asp Met Leu
85 90 95
Ala Leu Leu Gly Gln Glu Gln Thr Pro Arg Asp Phe Leu Val His Gln
100 105 110
Ala Gly Val Leu Gly Gly Leu Val Glu Val Leu Leu Gly Ala Leu Val
115 120 125
Pro Gly Gly Pro Pro Thr Pro Thr Arg Pro Pro Cys Thr Arg Asp Gly
130 135 140
Pro Ser Asp Cys Val Leu Ala Ala Asp Trp Leu Pro Ser Leu Leu Leu
145 150 155 160
Leu Leu Glu Gly Thr Arg Trp Gln Ala Leu Val Gln Val Gln Pro Ser
165 170 175
Val Asp Pro Thr Asn Ala Thr Gly Leu Asp Gly Arg Glu Ala Ala Pro
180 185 190
His Phe Leu Gln Gly Leu Leu Gly Leu Leu Thr Pro Thr Gly Glu Leu
195 200 205
Gly Ser Lys Glu Ala Leu Trp Gly Gly Leu Leu Arg Thr Val Gly Ala
210 215 220
Pro Leu Tyr Ala Ala Phe Gln Glu Gly Leu Leu Arg Val Thr His Ser
225 230 235 240
Leu Gln Asp Glu Val Phe Ser Ile Leu Gly Gln Pro Glu Pro Asp Thr
245 250 255
Asn Gly Gln Cys Gln Gly Gly Asn Leu Gln Gln Leu Leu Leu Trp Gly
260 265 270
Val Arg His Asn Leu Ser Trp Asp Val Gln Ala Leu Gly Phe Leu Ser
275 280 285
Gly Ser Pro Pro Pro Pro Pro Ala Leu Leu His Cys Leu Ser Thr Gly
290 295 300
Val Pro Leu Pro Arg Ala Ser Gln Pro Ser Ala His Ile Ser Pro Arg
305 310 315 320
Gln Arg Arg Ala Ile Thr Val Glu Ala Leu Cys Glu Asn His Leu Gly
325 330 335
Pro Ala Pro Pro Tyr Ser Ile Ser Asn Phe Ser Ile His Leu Leu Cys
340 345 350
Gln His Thr Lys Pro Ala Thr Pro Gln Pro His Pro Ser Thr Thr Ala
355 360 365
Ile Cys Gln Thr Ala Val Trp Tyr Ala Val Ser Trp Ala Pro Gly Ala
370 375 380
Gln Gly Trp Leu Gln Ala Cys His Asp Gln Phe Pro Asp Glu Phe Leu
385 390 395 400
Asp Ala Ile Cys Ser Asn Leu Ser Phe Ser Ala Leu Ser Gly Ser Asn
405 410 415
Arg Arg Leu Val Lys Arg Leu Cys Ala Gly Leu Leu Pro Pro Pro Thr
420 425 430
Ser Cys Pro Glu Gly Leu Pro Pro Val Pro Leu Thr Pro Asp Ile Phe
435 440 445
Trp Gly Cys Phe Leu Glu Asn Glu Thr Leu Trp Ala Glu Arg Leu Cys
450 455 460
Gly Glu Ala Ser Leu Gln Ala Val Pro Pro Ser Asn Gln Ala Trp Val
465 470 475 480
Gln His Val Cys Gln Gly Pro Thr Pro Asp Val Thr Ala Ser Pro Pro
485 490 495
Cys His Ile Gly Pro Cys Gly Glu Arg Cys Pro Asp Gly Gly Ser Phe
500 505 510
Leu Val Met Val Cys Ala Asn Asp Thr Met Tyr Glu Val Leu Val Pro
515 520 525
Phe Trp Pro Trp Leu Ala Gly Gln Cys Arg Ile Ser Arg Gly Gly Asn
530 535 540
Asp Thr Cys Phe Leu Glu Gly Leu Leu Gly Pro Leu Leu Pro Ser Leu
545 550 555 560
Pro Pro Leu Gly Pro Ser Pro Leu Cys Leu Thr Pro Gly Pro Phe Leu
565 570 575
Leu Gly Met Leu Ser Gln Leu Pro Arg Cys Gln Ser Ser Val Pro Ala
580 585 590
Leu Ala His Pro Thr Arg Leu His Tyr Leu Leu Arg Leu Leu Thr Phe
595 600 605
Leu Leu Gly Pro Gly Ala Gly Gly Ala Glu Ala Gln Gly Met Leu Gly
610 615 620
Arg Ala Leu Leu Leu Ser Ser Leu Pro Asp Asn Cys Ser Phe Trp Asp
625 630 635 640
Ala Phe Arg Pro Glu Gly Arg Arg Ser Val Leu Arg Thr Ile Gly Glu
645 650 655
Tyr Leu Glu Gln Asp Glu Glu Gln Pro Thr Pro Ser Gly Phe Glu Pro
660 665 670
Thr Val Asn Pro Ser Ser Gly Ile Ser Lys Met Glu Leu Leu Ala
675 680 685
<210> 16
<211> 724
<212> PRT
<213> Mus musculus
<400> 16
Ala Pro Thr Gly Pro Gln Ser Leu Asp Ala Gly Leu Ser Leu Leu Lys
1 5 10 15
Ser Phe Val Ala Thr Leu Asp Gln Ala Pro Gln Arg Ser Leu Ser Gln
20 25 30
Ser Arg Phe Ser Ala Phe Leu Ala Asn Ile Ser Ser Ser Phe Gln Leu
35 40 45
Gly Arg Met Gly Glu Gly Pro Val Gly Glu Pro Pro Pro Leu Gln Pro
50 55 60
Pro Ala Leu Arg Leu His Asp Phe Leu Val Thr Leu Arg Gly Ser Pro
65 70 75 80
Asp Trp Glu Pro Met Leu Gly Leu Leu Gly Asp Val Leu Ala Leu Leu
85 90 95
Gly Gln Glu Gln Thr Pro Arg Asp Phe Leu Val His Gln Ala Gly Val
100 105 110
Leu Gly Gly Leu Val Glu Ala Leu Leu Gly Ala Leu Val Pro Gly Gly
115 120 125
Pro Pro Ala Pro Thr Arg Pro Pro Cys Thr Arg Asp Gly Pro Ser Asp
130 135 140
Cys Val Leu Ala Ala Asp Trp Leu Pro Ser Leu Met Leu Leu Leu Glu
145 150 155 160
Gly Thr Arg Trp Gln Ala Leu Val Gln Leu Gln Pro Ser Val Asp Pro
165 170 175
Thr Asn Ala Thr Gly Leu Asp Gly Arg Glu Pro Ala Pro His Phe Leu
180 185 190
Gln Gly Leu Leu Gly Leu Leu Thr Pro Ala Gly Glu Leu Gly Ser Glu
195 200 205
Glu Ala Leu Trp Gly Gly Leu Leu Arg Thr Val Gly Ala Pro Leu Tyr
210 215 220
Ala Ala Phe Gln Glu Gly Leu Leu Arg Val Thr His Ser Leu Gln Asp
225 230 235 240
Glu Val Phe Ser Ile Met Gly Gln Pro Glu Pro Asp Ala Ser Gly Gln
245 250 255
Cys Gln Gly Gly Asn Leu Gln Gln Leu Leu Leu Trp Gly Met Arg Asn
260 265 270
Asn Leu Ser Trp Asp Ala Arg Ala Leu Gly Phe Leu Ser Gly Ser Pro
275 280 285
Pro Pro Pro Pro Ala Leu Leu His Cys Leu Ser Arg Gly Val Pro Leu
290 295 300
Pro Arg Ala Ser Gln Pro Ala Ala His Ile Ser Pro Arg Gln Arg Arg
305 310 315 320
Ala Ile Ser Val Glu Ala Leu Cys Glu Asn His Ser Gly Pro Glu Pro
325 330 335
Pro Tyr Ser Ile Ser Asn Phe Ser Ile Tyr Leu Leu Cys Gln His Ile
340 345 350
Lys Pro Ala Thr Pro Arg Pro Pro Pro Thr Thr Pro Arg Pro Pro Pro
355 360 365
Thr Thr Pro Gln Pro Pro Pro Thr Thr Thr Gln Pro Ile Pro Asp Thr
370 375 380
Thr Gln Pro Pro Pro Val Thr Pro Arg Pro Pro Pro Thr Thr Pro Gln
385 390 395 400
Pro Pro Pro Ser Thr Ala Val Ile Cys Gln Thr Ala Val Trp Tyr Ala
405 410 415
Val Ser Trp Ala Pro Gly Ala Arg Gly Trp Leu Gln Ala Cys His Asp
420 425 430
Gln Phe Pro Asp Gln Phe Leu Asp Met Ile Cys Gly Asn Leu Ser Phe
435 440 445
Ser Ala Leu Ser Gly Pro Ser Arg Pro Leu Val Lys Gln Leu Cys Ala
450 455 460
Gly Leu Leu Pro Pro Pro Thr Ser Cys Pro Pro Gly Leu Ile Pro Val
465 470 475 480
Pro Leu Thr Pro Glu Ile Phe Trp Gly Cys Phe Leu Glu Asn Glu Thr
485 490 495
Leu Trp Ala Glu Arg Leu Cys Val Glu Asp Ser Leu Gln Ala Val Pro
500 505 510
Pro Arg Asn Gln Ala Trp Val Gln His Val Cys Arg Gly Pro Thr Leu
515 520 525
Asp Ala Thr Asp Phe Pro Pro Cys Arg Val Gly Pro Cys Gly Glu Arg
530 535 540
Cys Pro Asp Gly Gly Ser Phe Leu Leu Met Val Cys Ala Asn Asp Thr
545 550 555 560
Leu Tyr Glu Ala Leu Val Pro Phe Trp Ala Trp Leu Ala Gly Gln Cys
565 570 575
Arg Ile Ser Arg Gly Gly Asn Asp Thr Cys Phe Leu Glu Gly Met Leu
580 585 590
Gly Pro Leu Leu Pro Ser Leu Pro Pro Leu Gly Pro Ser Pro Leu Cys
595 600 605
Leu Ala Pro Gly Pro Phe Leu Leu Gly Met Leu Ser Gln Leu Pro Arg
610 615 620
Cys Gln Ser Ser Val Pro Ala Leu Ala His Pro Thr Arg Leu His Tyr
625 630 635 640
Leu Leu Arg Leu Leu Thr Phe Leu Leu Gly Pro Gly Thr Gly Gly Ala
645 650 655
Glu Thr Gln Gly Met Leu Gly Gln Ala Leu Leu Leu Ser Ser Leu Pro
660 665 670
Asp Asn Cys Ser Phe Trp Asp Ala Phe Arg Pro Glu Gly Arg Arg Ser
675 680 685
Val Leu Arg Thr Val Gly Glu Tyr Leu Gln Arg Glu Glu Pro Thr Pro
690 695 700
Pro Gly Leu Asp Ser Ser Leu Ser Leu Gly Ser Gly Met Ser Lys Met
705 710 715 720
Glu Leu Leu Ser
<210> 17
<211> 3423
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 17
atggctctca gcctctggcc cctgctgctg ctgctgctgc tgctgctgct gctgtccttt 60
gcaatcaaga tagctacaag gaagtatctt ggcaaacaaa acgtttatga tattggagtc 120
gaaagagatc acaactttgc tctgaagaac ggattcatag cttctaattg ctttagtcct 180
gtgctgtggg atctgctcca gagggaaaag agtgtttggg ccctgcagat tctagtgcag 240
gcgtacctgc atatgccccc agaaaacctc cagcagctgg tgctttcagc agagagggag 300
gctgcacagg gcttcctgac actcatgctg caggggaagc tgcaggggaa gctgcaggta 360
ccaccatccg aggagcaggc cctgggtcgc ctgacagccc tgctgctcca gcggtaccca 420
cgcctcacct cccagctctt cattgacctg tcaccactca tccctttctt ggctgtctct 480
gacctgatgc gcttcccacc atccctgtta gccaacgaca gtgtcctggc tgccatccgg 540
gattacagcc caggaatgag gcctgaacag aaggaggctc tggcaaagcg actgctggcc 600
cctgaactgt ttggggaagt gcctgcctgg ccccaggagc tgctgtgggc agtgctgccc 660
ctgctccccc acctccctct ggagaacttt ttgcagctca gccctcacca gatccaggcc 720
ctggaggata gctggccagc agcaggtctg gggccagggc atgcccgcca tgtgctgcgc 780
agcctggtaa accagagtgt ccaggatggt gaggagcagg tacgcaggct tgggcccctc 840
gcctgtttcc tgagccctga ggagctgcag agcctagtgc ccctgagtga tccaacgggg 900
ccagtagaac gggggctgct ggaatgtgca gccaatggga ccctcagccc agaaggacgg 960
gtggcatatg aacttctggg tgtgttgcgc tcatctggag gagcggtgct gagcccccgg 1020
gagctgcggg tctgggcccc tctcttctct cagctgggcc tccgcttcct tcaggagctg 1080
tcagagcccc agcttagagc catgcttcct gtcctgcagg gaactagtgt tacacctgct 1140
caggctgtcc tgctgcttgg acggctcctt cctaggcacg atctatccct ggaggaactc 1200
tgctccttgc accttctgct accaggcctc agcccccaga cactccaggc catccctagg 1260
cgagtcctgg tcggggcttg ttcctgcctg gcccctgaac tgtcacgcct ctcagcctgc 1320
cagaccgcag cactgctgca gacctttcgg gttaaagatg gtgttaaaaa tatgggtaca 1380
acaggtgctg gtccagctgt gtgtatccct ggtcagccta ttcccaccac ctggccagac 1440
tgcctgcttc ccctgctccc attaaagctg ctacaactgg attccttggc tcttctggca 1500
aatcgaagac gctactggga gctgccctgg tctgagcagc aggcacagtt tctctggaag 1560
aagatgcaag tacccaccaa ccttaccctc aggaatctgc aggctctggg caccctggca 1620
ggaggcatgt cctgtgagtt tctgcagcag atcaactcca tggtagactt ccttgaagtg 1680
gtgcacatga tctatcagct gcccactaga gttcgaggga gcctgagggc ctgtatctgg 1740
gcagagctac agcggaggat ggcaatgcca gaaccagaat ggacaactgt agggccagaa 1800
ctgaacgggc tggatagcaa gctactcctg gacttaccga tccagttgat ggacagacta 1860
tccaatgaat ccattatgtt ggtggtggag ctggtgcaaa gagctccaga gcagctgctg 1920
gcactgaccc ccctccacca ggcagccctg gcagagaggg cactacaaaa cctggctcca 1980
aaggagactc cagtctcagg ggaagtgctg gagaccttag gccctttggt tggattcctg 2040
gggacagaga gcacacgaca gatcccccta cagatcctgc tgtcccatct cagtcagctg 2100
caaggcttct gcctaggaga gacatttgcc acagagctgg gatggctgct attgcaggag 2160
tctgttcttg ggaaaccaga gttgtggagc caggatgaag tagagcaagc tggacgccta 2220
gtattcactc tgtctactga ggcaatttcc ttgatcccca gggaggcctt gggtccagag 2280
accctggagc ggcttctaga aaagcagcag agctgggagc agagcagagt tggacagctg 2340
tgtagggagc cacagcttgc tgccaagaaa gcagccctgg tagcaggggt ggtgcgacca 2400
gctgctgagg atcttccaga acctgtgcca aattgtgcag atgtacgagg gacattccca 2460
gcagcctggt ctgcaaccca gattgcagag atggagctct cagactttga ggactgcctg 2520
acattatttg caggagaccc aggacttggg cctgaggaac tgcgggcagc catgggcaaa 2580
gcaaaacagt tgtggggtcc cccccgggga tttcgtcctg agcagatcct gcagcttggt 2640
aggctcttaa taggtctagg agatcgggaa ctacaggagc tgatcctagt ggactgggga 2700
gtgctgagca ccctggggca gatagatggc tggagcacca ctcagctccg cattgtggtc 2760
tccagtttcc tacggcagag tggtcggcat gtgagccacc tggacttcgt tcatctgaca 2820
gcgctgggtt atactctctg tggactgcgg ccagaggagc tccagcacat cagcagttgg 2880
gagttcagcc aagcagctct cttcctcggc accctgcatc tccagtgctc tgaggaacaa 2940
ctggaggttc tggcccacct acttgtactg cctggtgggt ttggcccaat cagtaactgg 3000
gggcctgaga tcttcactga aattggcacc atagcagctg ggatcccaga cctggctctt 3060
tcagcactgc tgcggggaca gatccagggc gttactcctc ttgccatttc tgtcatccct 3120
cctcctaaat ttgctgtggt gtttagtccc atccaactat ctagtctcac cagtgctcag 3180
gctgtggctg tcactcctga gcaaatggcc tttctgagtc ctgagcagcg acgagcagtt 3240
gcatgggccc aacatgaggg aaaggagagc ccagaacagc aaggtcgaag tacagcctgg 3300
ggcctccagg actggtcacg accttcctgg tccctggtat tgactatcag cttccttggc 3360
cacctgctaa cgcgtacgcg gccgctcgag cagaaactca tctcagaaga ggatctgtaa 3420
tag 3423
<210> 18
<211> 1139
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 18
Met Ala Leu Ser Leu Trp Pro Leu Leu Leu Leu Leu Leu Leu Leu Leu
1 5 10 15
Leu Leu Ser Phe Ala Ile Lys Ile Ala Thr Arg Lys Tyr Leu Gly Lys
20 25 30
Gln Asn Val Tyr Asp Ile Gly Val Glu Arg Asp His Asn Phe Ala Leu
35 40 45
Lys Asn Gly Phe Ile Ala Ser Asn Cys Phe Ser Pro Val Leu Trp Asp
50 55 60
Leu Leu Gln Arg Glu Lys Ser Val Trp Ala Leu Gln Ile Leu Val Gln
65 70 75 80
Ala Tyr Leu His Met Pro Pro Glu Asn Leu Gln Gln Leu Val Leu Ser
85 90 95
Ala Glu Arg Glu Ala Ala Gln Gly Phe Leu Thr Leu Met Leu Gln Gly
100 105 110
Lys Leu Gln Gly Lys Leu Gln Val Pro Pro Ser Glu Glu Gln Ala Leu
115 120 125
Gly Arg Leu Thr Ala Leu Leu Leu Gln Arg Tyr Pro Arg Leu Thr Ser
130 135 140
Gln Leu Phe Ile Asp Leu Ser Pro Leu Ile Pro Phe Leu Ala Val Ser
145 150 155 160
Asp Leu Met Arg Phe Pro Pro Ser Leu Leu Ala Asn Asp Ser Val Leu
165 170 175
Ala Ala Ile Arg Asp Tyr Ser Pro Gly Met Arg Pro Glu Gln Lys Glu
180 185 190
Ala Leu Ala Lys Arg Leu Leu Ala Pro Glu Leu Phe Gly Glu Val Pro
195 200 205
Ala Trp Pro Gln Glu Leu Leu Trp Ala Val Leu Pro Leu Leu Pro His
210 215 220
Leu Pro Leu Glu Asn Phe Leu Gln Leu Ser Pro His Gln Ile Gln Ala
225 230 235 240
Leu Glu Asp Ser Trp Pro Ala Ala Gly Leu Gly Pro Gly His Ala Arg
245 250 255
His Val Leu Arg Ser Leu Val Asn Gln Ser Val Gln Asp Gly Glu Glu
260 265 270
Gln Val Arg Arg Leu Gly Pro Leu Ala Cys Phe Leu Ser Pro Glu Glu
275 280 285
Leu Gln Ser Leu Val Pro Leu Ser Asp Pro Thr Gly Pro Val Glu Arg
290 295 300
Gly Leu Leu Glu Cys Ala Ala Asn Gly Thr Leu Ser Pro Glu Gly Arg
305 310 315 320
Val Ala Tyr Glu Leu Leu Gly Val Leu Arg Ser Ser Gly Gly Ala Val
325 330 335
Leu Ser Pro Arg Glu Leu Arg Val Trp Ala Pro Leu Phe Ser Gln Leu
340 345 350
Gly Leu Arg Phe Leu Gln Glu Leu Ser Glu Pro Gln Leu Arg Ala Met
355 360 365
Leu Pro Val Leu Gln Gly Thr Ser Val Thr Pro Ala Gln Ala Val Leu
370 375 380
Leu Leu Gly Arg Leu Leu Pro Arg His Asp Leu Ser Leu Glu Glu Leu
385 390 395 400
Cys Ser Leu His Leu Leu Leu Pro Gly Leu Ser Pro Gln Thr Leu Gln
405 410 415
Ala Ile Pro Arg Arg Val Leu Val Gly Ala Cys Ser Cys Leu Ala Pro
420 425 430
Glu Leu Ser Arg Leu Ser Ala Cys Gln Thr Ala Ala Leu Leu Gln Thr
435 440 445
Phe Arg Val Lys Asp Gly Val Lys Asn Met Gly Thr Thr Gly Ala Gly
450 455 460
Pro Ala Val Cys Ile Pro Gly Gln Pro Ile Pro Thr Thr Trp Pro Asp
465 470 475 480
Cys Leu Leu Pro Leu Leu Pro Leu Lys Leu Leu Gln Leu Asp Ser Leu
485 490 495
Ala Leu Leu Ala Asn Arg Arg Arg Tyr Trp Glu Leu Pro Trp Ser Glu
500 505 510
Gln Gln Ala Gln Phe Leu Trp Lys Lys Met Gln Val Pro Thr Asn Leu
515 520 525
Thr Leu Arg Asn Leu Gln Ala Leu Gly Thr Leu Ala Gly Gly Met Ser
530 535 540
Cys Glu Phe Leu Gln Gln Ile Asn Ser Met Val Asp Phe Leu Glu Val
545 550 555 560
Val His Met Ile Tyr Gln Leu Pro Thr Arg Val Arg Gly Ser Leu Arg
565 570 575
Ala Cys Ile Trp Ala Glu Leu Gln Arg Arg Met Ala Met Pro Glu Pro
580 585 590
Glu Trp Thr Thr Val Gly Pro Glu Leu Asn Gly Leu Asp Ser Lys Leu
595 600 605
Leu Leu Asp Leu Pro Ile Gln Leu Met Asp Arg Leu Ser Asn Glu Ser
610 615 620
Ile Met Leu Val Val Glu Leu Val Gln Arg Ala Pro Glu Gln Leu Leu
625 630 635 640
Ala Leu Thr Pro Leu His Gln Ala Ala Leu Ala Glu Arg Ala Leu Gln
645 650 655
Asn Leu Ala Pro Lys Glu Thr Pro Val Ser Gly Glu Val Leu Glu Thr
660 665 670
Leu Gly Pro Leu Val Gly Phe Leu Gly Thr Glu Ser Thr Arg Gln Ile
675 680 685
Pro Leu Gln Ile Leu Leu Ser His Leu Ser Gln Leu Gln Gly Phe Cys
690 695 700
Leu Gly Glu Thr Phe Ala Thr Glu Leu Gly Trp Leu Leu Leu Gln Glu
705 710 715 720
Ser Val Leu Gly Lys Pro Glu Leu Trp Ser Gln Asp Glu Val Glu Gln
725 730 735
Ala Gly Arg Leu Val Phe Thr Leu Ser Thr Glu Ala Ile Ser Leu Ile
740 745 750
Pro Arg Glu Ala Leu Gly Pro Glu Thr Leu Glu Arg Leu Leu Glu Lys
755 760 765
Gln Gln Ser Trp Glu Gln Ser Arg Val Gly Gln Leu Cys Arg Glu Pro
770 775 780
Gln Leu Ala Ala Lys Lys Ala Ala Leu Val Ala Gly Val Val Arg Pro
785 790 795 800
Ala Ala Glu Asp Leu Pro Glu Pro Val Pro Asn Cys Ala Asp Val Arg
805 810 815
Gly Thr Phe Pro Ala Ala Trp Ser Ala Thr Gln Ile Ala Glu Met Glu
820 825 830
Leu Ser Asp Phe Glu Asp Cys Leu Thr Leu Phe Ala Gly Asp Pro Gly
835 840 845
Leu Gly Pro Glu Glu Leu Arg Ala Ala Met Gly Lys Ala Lys Gln Leu
850 855 860
Trp Gly Pro Pro Arg Gly Phe Arg Pro Glu Gln Ile Leu Gln Leu Gly
865 870 875 880
Arg Leu Leu Ile Gly Leu Gly Asp Arg Glu Leu Gln Glu Leu Ile Leu
885 890 895
Val Asp Trp Gly Val Leu Ser Thr Leu Gly Gln Ile Asp Gly Trp Ser
900 905 910
Thr Thr Gln Leu Arg Ile Val Val Ser Ser Phe Leu Arg Gln Ser Gly
915 920 925
Arg His Val Ser His Leu Asp Phe Val His Leu Thr Ala Leu Gly Tyr
930 935 940
Thr Leu Cys Gly Leu Arg Pro Glu Glu Leu Gln His Ile Ser Ser Trp
945 950 955 960
Glu Phe Ser Gln Ala Ala Leu Phe Leu Gly Thr Leu His Leu Gln Cys
965 970 975
Ser Glu Glu Gln Leu Glu Val Leu Ala His Leu Leu Val Leu Pro Gly
980 985 990
Gly Phe Gly Pro Ile Ser Asn Trp Gly Pro Glu Ile Phe Thr Glu Ile
995 1000 1005
Gly Thr Ile Ala Ala Gly Ile Pro Asp Leu Ala Leu Ser Ala Leu
1010 1015 1020
Leu Arg Gly Gln Ile Gln Gly Val Thr Pro Leu Ala Ile Ser Val
1025 1030 1035
Ile Pro Pro Pro Lys Phe Ala Val Val Phe Ser Pro Ile Gln Leu
1040 1045 1050
Ser Ser Leu Thr Ser Ala Gln Ala Val Ala Val Thr Pro Glu Gln
1055 1060 1065
Met Ala Phe Leu Ser Pro Glu Gln Arg Arg Ala Val Ala Trp Ala
1070 1075 1080
Gln His Glu Gly Lys Glu Ser Pro Glu Gln Gln Gly Arg Ser Thr
1085 1090 1095
Ala Trp Gly Leu Gln Asp Trp Ser Arg Pro Ser Trp Ser Leu Val
1100 1105 1110
Leu Thr Ile Ser Phe Leu Gly His Leu Leu Thr Arg Thr Arg Pro
1115 1120 1125
Leu Glu Gln Lys Leu Ile Ser Glu Glu Asp Leu
1130 1135
<210> 19
<211> 3414
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 19
atggctctga gcctccagcc ccagctgctc cttctcctgt cgctcctgcc gcaggaagtg 60
acttcaatca agatagctac aaggaagtat cttggcaaac aaaacgttta tgatattgga 120
gtcgaaagag atcacaactt tgctctgaag aacggattca tagcttctaa ttgcttcagt 180
cctgtactgt gggatctact ccagagagag aagagcgttt gggccctgag gaccctggtg 240
aaggcctacc tgcgcatgcc tccagaagac cttcagcagc ttgtgctttc agcagagatg 300
gaggctgcac agggcttcct gacgctcatg cttcgttcct gggctaagct gaaggttcaa 360
ccatccgagg agcaggccat gggccgcctg acagccttgc tgctccagcg gtacccacgc 420
ctcacctccc aactctttat cgacatgtca ccgctcatcc ccttcctggc tgtccctgac 480
ctcatgcgct tcccaccgtc ccttttggcc aacgacagtg tcctggctgc catcagggat 540
cacagctcag gaatgaagcc tgaacagaag gaggccctgg caaaacgact gctggcccct 600
gagctgtttg gagaagtgcc tgattggccc caggagctgc tgtgggcagc cctgcctctg 660
cttccccatc tgcctctgga gagctttctc cagctcagcc ctcaccagat ccaggccctg 720
gaggatagct ggccagtagc agatcttggg ccgggacacg cccgacatgt gcttcgtagc 780
ctagtaaacc agagcatgga ggatggggag gagcaggtgc tcaggcttgg gtccctcgcc 840
tgtttcctga gtcctgagga gctacagagt ctggtgccct tgagtgatcc aatggggcct 900
gtagaacagg gtctgctgga atgtgcggcc aatgggaccc tcagcccaga aggacgggtg 960
gcatatgaac ttctgggagt gttgcgttca tctggaggaa ctgtcttaag cccccgagag 1020
ctgagggtct gggcacctct ctttccccag ctgggcctcc gcttcctgca ggagctctca 1080
gagacccagc ttagagccat gcttcctgcc ctacagggag ccagtgtcac acctgcccag 1140
gctgttctgt tgtttggaag gctccttcct aagcatgatc tgtccctgga ggaactctgc 1200
tccctgcacc ctctcctgcc aggtctcagc ccccagacac tccaggccat ccctaagaga 1260
gttctggttg gtgcttgttc ctgcctgggc cctgaactgt caaggctttc agcttgccag 1320
attgcagctc tgctgcagac ctttcgggta aaagatggtg ttaaaaatat gggtgcagca 1380
ggtgccggct cagccgtgtg cattcctggg cagcccacca cttggccaga ctgcctgctt 1440
cccctgctcc cattaaagct gctacagctg gacgctgcag ctcttctggc aaaccgaaga 1500
ctctatcggc agctgccttg gtctgagcaa caggcacagt ttctctggaa gaaaatgcaa 1560
gtgcctacca acctgagcct gaggaatctg caggctctgg gcaacttggc aggaggcatg 1620
acctgcgagt ttctgcagca gatcagctca atggttgact ttcttgatgt ggtacacatg 1680
ctctaccagc tgcccactgg tgttcgagag agcctgcggg cctgtatctg gacagagcta 1740
cagcggagga tgacaatgcc agagccagag ctgaccaccc tagggccaga actgagtgaa 1800
cttgacacaa agctactcct ggacttgccg atccagctga tggacagatt gtccaatgat 1860
tccattatgt tggtggtgga gatggtccaa ggcgctccag agcagctgct ggcactgacc 1920
ccactccacc agacagcctt ggcagagcga gcacttaaaa acctggctcc aaaggagacc 1980
ccaatctcca aagaagtgct ggagacactg ggccccttgg ttggattcct gggaatagag 2040
agcacgcgac ggatcccttt acccattcta ctgtctcatc tcagtcagct gcagggcttc 2100
tgcctaggag agacatttgc cacagagctg ggatggctgc tgttgcagga gcctgttctt 2160
ggaaaaccag aattgtggag ccaggatgaa atagagcaag ctggacgcct agtattcact 2220
ctgtctgctg aggctatttc ctcgatcccc agggaggctt tgggcccaga gacactggag 2280
aggcttctgg gaaagcatca aagctgggag cagagcagag tgggccatct gtgtggggag 2340
tcacagcttg cccacaagaa agcagctctg gtagctggga ttgtgcatcc agctgctgag 2400
ggtctccaag agcctgtacc aaactgtgca gacatacggg gaaccttccc agcggcctgg 2460
tctgcgacac aaatctcaga gatggaactc tcagactttg aagactgcct gtcactattt 2520
gctggagatc caggacttgg tcctgaggaa ctacgggcag ccatgggcaa ggccaagcag 2580
ttgtggggtc cccctcgagg attccgtcct gagcagatct tgcagctggg ccgtctcctg 2640
ataggtctag gagaacggga actgcaggag cttaccttgg tggactgggg tgtgctgagc 2700
agcctggggc aaatagatgg ctggagttcc atgcagctcc gagccgtggt ctccagtttc 2760
ctaaggcaga gtggtcggca tgtgagccac ctggacttca tttatctgac agcactgggt 2820
tacacagtct gtggattgcg accagaggag ttacagcaca tcagcagttg ggagtttagc 2880
caagcagctc tcttcctggg tagcttgcat ctcccgtgct ctgaggaaca gctggaagtt 2940
ctggcctatc tccttgtgtt gcctggtggc tttggcccag tcagtaactg ggggcctgag 3000
atcttcactg aaattggcac aatagcagct ggcatcccag acctggctct ttcagcatta 3060
ctgcggggac agatccaagg cctgactcct cttgccattt ctgtcattcc tgctcccaag 3120
tttgcagtgg tcttcaaccc catccagtta tctagtctca ccaggggtca ggccgtagct 3180
gttactcctg aacagctggc ctatctgagt cctgagcagc ggcgagcagt tgcatgggcc 3240
caacacgaag ggaaggagat cccagagcag ctgggtcgaa actcagcctg gggtctctac 3300
gactggttcc aagcctcctg ggccctggca ttgcccgtca gcatttttgg ccacctatta 3360
acgcgtacgc ggccgctcga gcagaaactc atctcagaag aggatctgta atag 3414
<210> 20
<211> 1136
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 20
Met Ala Leu Ser Leu Gln Pro Gln Leu Leu Leu Leu Leu Ser Leu Leu
1 5 10 15
Pro Gln Glu Val Thr Ser Ile Lys Ile Ala Thr Arg Lys Tyr Leu Gly
20 25 30
Lys Gln Asn Val Tyr Asp Ile Gly Val Glu Arg Asp His Asn Phe Ala
35 40 45
Leu Lys Asn Gly Phe Ile Ala Ser Asn Cys Phe Ser Pro Val Leu Trp
50 55 60
Asp Leu Leu Gln Arg Glu Lys Ser Val Trp Ala Leu Arg Thr Leu Val
65 70 75 80
Lys Ala Tyr Leu Arg Met Pro Pro Glu Asp Leu Gln Gln Leu Val Leu
85 90 95
Ser Ala Glu Met Glu Ala Ala Gln Gly Phe Leu Thr Leu Met Leu Arg
100 105 110
Ser Trp Ala Lys Leu Lys Val Gln Pro Ser Glu Glu Gln Ala Met Gly
115 120 125
Arg Leu Thr Ala Leu Leu Leu Gln Arg Tyr Pro Arg Leu Thr Ser Gln
130 135 140
Leu Phe Ile Asp Met Ser Pro Leu Ile Pro Phe Leu Ala Val Pro Asp
145 150 155 160
Leu Met Arg Phe Pro Pro Ser Leu Leu Ala Asn Asp Ser Val Leu Ala
165 170 175
Ala Ile Arg Asp His Ser Ser Gly Met Lys Pro Glu Gln Lys Glu Ala
180 185 190
Leu Ala Lys Arg Leu Leu Ala Pro Glu Leu Phe Gly Glu Val Pro Asp
195 200 205
Trp Pro Gln Glu Leu Leu Trp Ala Ala Leu Pro Leu Leu Pro His Leu
210 215 220
Pro Leu Glu Ser Phe Leu Gln Leu Ser Pro His Gln Ile Gln Ala Leu
225 230 235 240
Glu Asp Ser Trp Pro Val Ala Asp Leu Gly Pro Gly His Ala Arg His
245 250 255
Val Leu Arg Ser Leu Val Asn Gln Ser Met Glu Asp Gly Glu Glu Gln
260 265 270
Val Leu Arg Leu Gly Ser Leu Ala Cys Phe Leu Ser Pro Glu Glu Leu
275 280 285
Gln Ser Leu Val Pro Leu Ser Asp Pro Met Gly Pro Val Glu Gln Gly
290 295 300
Leu Leu Glu Cys Ala Ala Asn Gly Thr Leu Ser Pro Glu Gly Arg Val
305 310 315 320
Ala Tyr Glu Leu Leu Gly Val Leu Arg Ser Ser Gly Gly Thr Val Leu
325 330 335
Ser Pro Arg Glu Leu Arg Val Trp Ala Pro Leu Phe Pro Gln Leu Gly
340 345 350
Leu Arg Phe Leu Gln Glu Leu Ser Glu Thr Gln Leu Arg Ala Met Leu
355 360 365
Pro Ala Leu Gln Gly Ala Ser Val Thr Pro Ala Gln Ala Val Leu Leu
370 375 380
Phe Gly Arg Leu Leu Pro Lys His Asp Leu Ser Leu Glu Glu Leu Cys
385 390 395 400
Ser Leu His Pro Leu Leu Pro Gly Leu Ser Pro Gln Thr Leu Gln Ala
405 410 415
Ile Pro Lys Arg Val Leu Val Gly Ala Cys Ser Cys Leu Gly Pro Glu
420 425 430
Leu Ser Arg Leu Ser Ala Cys Gln Ile Ala Ala Leu Leu Gln Thr Phe
435 440 445
Arg Val Lys Asp Gly Val Lys Asn Met Gly Ala Ala Gly Ala Gly Ser
450 455 460
Ala Val Cys Ile Pro Gly Gln Pro Thr Thr Trp Pro Asp Cys Leu Leu
465 470 475 480
Pro Leu Leu Pro Leu Lys Leu Leu Gln Leu Asp Ala Ala Ala Leu Leu
485 490 495
Ala Asn Arg Arg Leu Tyr Arg Gln Leu Pro Trp Ser Glu Gln Gln Ala
500 505 510
Gln Phe Leu Trp Lys Lys Met Gln Val Pro Thr Asn Leu Ser Leu Arg
515 520 525
Asn Leu Gln Ala Leu Gly Asn Leu Ala Gly Gly Met Thr Cys Glu Phe
530 535 540
Leu Gln Gln Ile Ser Ser Met Val Asp Phe Leu Asp Val Val His Met
545 550 555 560
Leu Tyr Gln Leu Pro Thr Gly Val Arg Glu Ser Leu Arg Ala Cys Ile
565 570 575
Trp Thr Glu Leu Gln Arg Arg Met Thr Met Pro Glu Pro Glu Leu Thr
580 585 590
Thr Leu Gly Pro Glu Leu Ser Glu Leu Asp Thr Lys Leu Leu Leu Asp
595 600 605
Leu Pro Ile Gln Leu Met Asp Arg Leu Ser Asn Asp Ser Ile Met Leu
610 615 620
Val Val Glu Met Val Gln Gly Ala Pro Glu Gln Leu Leu Ala Leu Thr
625 630 635 640
Pro Leu His Gln Thr Ala Leu Ala Glu Arg Ala Leu Lys Asn Leu Ala
645 650 655
Pro Lys Glu Thr Pro Ile Ser Lys Glu Val Leu Glu Thr Leu Gly Pro
660 665 670
Leu Val Gly Phe Leu Gly Ile Glu Ser Thr Arg Arg Ile Pro Leu Pro
675 680 685
Ile Leu Leu Ser His Leu Ser Gln Leu Gln Gly Phe Cys Leu Gly Glu
690 695 700
Thr Phe Ala Thr Glu Leu Gly Trp Leu Leu Leu Gln Glu Pro Val Leu
705 710 715 720
Gly Lys Pro Glu Leu Trp Ser Gln Asp Glu Ile Glu Gln Ala Gly Arg
725 730 735
Leu Val Phe Thr Leu Ser Ala Glu Ala Ile Ser Ser Ile Pro Arg Glu
740 745 750
Ala Leu Gly Pro Glu Thr Leu Glu Arg Leu Leu Gly Lys His Gln Ser
755 760 765
Trp Glu Gln Ser Arg Val Gly His Leu Cys Gly Glu Ser Gln Leu Ala
770 775 780
His Lys Lys Ala Ala Leu Val Ala Gly Ile Val His Pro Ala Ala Glu
785 790 795 800
Gly Leu Gln Glu Pro Val Pro Asn Cys Ala Asp Ile Arg Gly Thr Phe
805 810 815
Pro Ala Ala Trp Ser Ala Thr Gln Ile Ser Glu Met Glu Leu Ser Asp
820 825 830
Phe Glu Asp Cys Leu Ser Leu Phe Ala Gly Asp Pro Gly Leu Gly Pro
835 840 845
Glu Glu Leu Arg Ala Ala Met Gly Lys Ala Lys Gln Leu Trp Gly Pro
850 855 860
Pro Arg Gly Phe Arg Pro Glu Gln Ile Leu Gln Leu Gly Arg Leu Leu
865 870 875 880
Ile Gly Leu Gly Glu Arg Glu Leu Gln Glu Leu Thr Leu Val Asp Trp
885 890 895
Gly Val Leu Ser Ser Leu Gly Gln Ile Asp Gly Trp Ser Ser Met Gln
900 905 910
Leu Arg Ala Val Val Ser Ser Phe Leu Arg Gln Ser Gly Arg His Val
915 920 925
Ser His Leu Asp Phe Ile Tyr Leu Thr Ala Leu Gly Tyr Thr Val Cys
930 935 940
Gly Leu Arg Pro Glu Glu Leu Gln His Ile Ser Ser Trp Glu Phe Ser
945 950 955 960
Gln Ala Ala Leu Phe Leu Gly Ser Leu His Leu Pro Cys Ser Glu Glu
965 970 975
Gln Leu Glu Val Leu Ala Tyr Leu Leu Val Leu Pro Gly Gly Phe Gly
980 985 990
Pro Val Ser Asn Trp Gly Pro Glu Ile Phe Thr Glu Ile Gly Thr Ile
995 1000 1005
Ala Ala Gly Ile Pro Asp Leu Ala Leu Ser Ala Leu Leu Arg Gly
1010 1015 1020
Gln Ile Gln Gly Leu Thr Pro Leu Ala Ile Ser Val Ile Pro Ala
1025 1030 1035
Pro Lys Phe Ala Val Val Phe Asn Pro Ile Gln Leu Ser Ser Leu
1040 1045 1050
Thr Arg Gly Gln Ala Val Ala Val Thr Pro Glu Gln Leu Ala Tyr
1055 1060 1065
Leu Ser Pro Glu Gln Arg Arg Ala Val Ala Trp Ala Gln His Glu
1070 1075 1080
Gly Lys Glu Ile Pro Glu Gln Leu Gly Arg Asn Ser Ala Trp Gly
1085 1090 1095
Leu Tyr Asp Trp Phe Gln Ala Ser Trp Ala Leu Ala Leu Pro Val
1100 1105 1110
Ser Ile Phe Gly His Leu Leu Thr Arg Thr Arg Pro Leu Glu Gln
1115 1120 1125
Lys Leu Ile Ser Glu Glu Asp Leu
1130 1135
<210> 21
<211> 105
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 21
atcaagatag ctacaaggaa gtatcttggc aaacaaaacg tttatgatat tggagtcgaa 60
agagatcaca actttgctct gaagaacgga ttcatagctt ctaat 105
<210> 22
<211> 35
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 22
Ile Lys Ile Ala Thr Arg Lys Tyr Leu Gly Lys Gln Asn Val Tyr Asp
1 5 10 15
Ile Gly Val Glu Arg Asp His Asn Phe Ala Leu Lys Asn Gly Phe Ile
20 25 30
Ala Ser Asn
35
<210> 23
<211> 1067
<212> PRT
<213> Homo sapiens
<400> 23
Cys Phe Ser Pro Val Leu Trp Asp Leu Leu Gln Arg Glu Lys Ser Val
1 5 10 15
Trp Ala Leu Gln Ile Leu Val Gln Ala Tyr Leu His Met Pro Pro Glu
20 25 30
Asn Leu Gln Gln Leu Val Leu Ser Ala Glu Arg Glu Ala Ala Gln Gly
35 40 45
Phe Leu Thr Leu Met Leu Gln Gly Lys Leu Gln Gly Lys Leu Gln Val
50 55 60
Pro Pro Ser Glu Glu Gln Ala Leu Gly Arg Leu Thr Ala Leu Leu Leu
65 70 75 80
Gln Arg Tyr Pro Arg Leu Thr Ser Gln Leu Phe Ile Asp Leu Ser Pro
85 90 95
Leu Ile Pro Phe Leu Ala Val Ser Asp Leu Met Arg Phe Pro Pro Ser
100 105 110
Leu Leu Ala Asn Asp Ser Val Leu Ala Ala Ile Arg Asp Tyr Ser Pro
115 120 125
Gly Met Arg Pro Glu Gln Lys Glu Ala Leu Ala Lys Arg Leu Leu Ala
130 135 140
Pro Glu Leu Phe Gly Glu Val Pro Ala Trp Pro Gln Glu Leu Leu Trp
145 150 155 160
Ala Val Leu Pro Leu Leu Pro His Leu Pro Leu Glu Asn Phe Leu Gln
165 170 175
Leu Ser Pro His Gln Ile Gln Ala Leu Glu Asp Ser Trp Pro Ala Ala
180 185 190
Gly Leu Gly Pro Gly His Ala Arg His Val Leu Arg Ser Leu Val Asn
195 200 205
Gln Ser Val Gln Asp Gly Glu Glu Gln Val Arg Arg Leu Gly Pro Leu
210 215 220
Ala Cys Phe Leu Ser Pro Glu Glu Leu Gln Ser Leu Val Pro Leu Ser
225 230 235 240
Asp Pro Thr Gly Pro Val Glu Arg Gly Leu Leu Glu Cys Ala Ala Asn
245 250 255
Gly Thr Leu Ser Pro Glu Gly Arg Val Ala Tyr Glu Leu Leu Gly Val
260 265 270
Leu Arg Ser Ser Gly Gly Ala Val Leu Ser Pro Arg Glu Leu Arg Val
275 280 285
Trp Ala Pro Leu Phe Ser Gln Leu Gly Leu Arg Phe Leu Gln Glu Leu
290 295 300
Ser Glu Pro Gln Leu Arg Ala Met Leu Pro Val Leu Gln Gly Thr Ser
305 310 315 320
Val Thr Pro Ala Gln Ala Val Leu Leu Leu Gly Arg Leu Leu Pro Arg
325 330 335
His Asp Leu Ser Leu Glu Glu Leu Cys Ser Leu His Leu Leu Leu Pro
340 345 350
Gly Leu Ser Pro Gln Thr Leu Gln Ala Ile Pro Arg Arg Val Leu Val
355 360 365
Gly Ala Cys Ser Cys Leu Ala Pro Glu Leu Ser Arg Leu Ser Ala Cys
370 375 380
Gln Thr Ala Ala Leu Leu Gln Thr Phe Arg Val Lys Asp Gly Val Lys
385 390 395 400
Asn Met Gly Thr Thr Gly Ala Gly Pro Ala Val Cys Ile Pro Gly Gln
405 410 415
Pro Ile Pro Thr Thr Trp Pro Asp Cys Leu Leu Pro Leu Leu Pro Leu
420 425 430
Lys Leu Leu Gln Leu Asp Ser Leu Ala Leu Leu Ala Asn Arg Arg Arg
435 440 445
Tyr Trp Glu Leu Pro Trp Ser Glu Gln Gln Ala Gln Phe Leu Trp Lys
450 455 460
Lys Met Gln Val Pro Thr Asn Leu Thr Leu Arg Asn Leu Gln Ala Leu
465 470 475 480
Gly Thr Leu Ala Gly Gly Met Ser Cys Glu Phe Leu Gln Gln Ile Asn
485 490 495
Ser Met Val Asp Phe Leu Glu Val Val His Met Ile Tyr Gln Leu Pro
500 505 510
Thr Arg Val Arg Gly Ser Leu Arg Ala Cys Ile Trp Ala Glu Leu Gln
515 520 525
Arg Arg Met Ala Met Pro Glu Pro Glu Trp Thr Thr Val Gly Pro Glu
530 535 540
Leu Asn Gly Leu Asp Ser Lys Leu Leu Leu Asp Leu Pro Ile Gln Leu
545 550 555 560
Met Asp Arg Leu Ser Asn Glu Ser Ile Met Leu Val Val Glu Leu Val
565 570 575
Gln Arg Ala Pro Glu Gln Leu Leu Ala Leu Thr Pro Leu His Gln Ala
580 585 590
Ala Leu Ala Glu Arg Ala Leu Gln Asn Leu Ala Pro Lys Glu Thr Pro
595 600 605
Val Ser Gly Glu Val Leu Glu Thr Leu Gly Pro Leu Val Gly Phe Leu
610 615 620
Gly Thr Glu Ser Thr Arg Gln Ile Pro Leu Gln Ile Leu Leu Ser His
625 630 635 640
Leu Ser Gln Leu Gln Gly Phe Cys Leu Gly Glu Thr Phe Ala Thr Glu
645 650 655
Leu Gly Trp Leu Leu Leu Gln Glu Ser Val Leu Gly Lys Pro Glu Leu
660 665 670
Trp Ser Gln Asp Glu Val Glu Gln Ala Gly Arg Leu Val Phe Thr Leu
675 680 685
Ser Thr Glu Ala Ile Ser Leu Ile Pro Arg Glu Ala Leu Gly Pro Glu
690 695 700
Thr Leu Glu Arg Leu Leu Glu Lys Gln Gln Ser Trp Glu Gln Ser Arg
705 710 715 720
Val Gly Gln Leu Cys Arg Glu Pro Gln Leu Ala Ala Lys Lys Ala Ala
725 730 735
Leu Val Ala Gly Val Val Arg Pro Ala Ala Glu Asp Leu Pro Glu Pro
740 745 750
Val Pro Asn Cys Ala Asp Val Arg Gly Thr Phe Pro Ala Ala Trp Ser
755 760 765
Ala Thr Gln Ile Ala Glu Met Glu Leu Ser Asp Phe Glu Asp Cys Leu
770 775 780
Thr Leu Phe Ala Gly Asp Pro Gly Leu Gly Pro Glu Glu Leu Arg Ala
785 790 795 800
Ala Met Gly Lys Ala Lys Gln Leu Trp Gly Pro Pro Arg Gly Phe Arg
805 810 815
Pro Glu Gln Ile Leu Gln Leu Gly Arg Leu Leu Ile Gly Leu Gly Asp
820 825 830
Arg Glu Leu Gln Glu Leu Ile Leu Val Asp Trp Gly Val Leu Ser Thr
835 840 845
Leu Gly Gln Ile Asp Gly Trp Ser Thr Thr Gln Leu Arg Ile Val Val
850 855 860
Ser Ser Phe Leu Arg Gln Ser Gly Arg His Val Ser His Leu Asp Phe
865 870 875 880
Val His Leu Thr Ala Leu Gly Tyr Thr Leu Cys Gly Leu Arg Pro Glu
885 890 895
Glu Leu Gln His Ile Ser Ser Trp Glu Phe Ser Gln Ala Ala Leu Phe
900 905 910
Leu Gly Thr Leu His Leu Gln Cys Ser Glu Glu Gln Leu Glu Val Leu
915 920 925
Ala His Leu Leu Val Leu Pro Gly Gly Phe Gly Pro Ile Ser Asn Trp
930 935 940
Gly Pro Glu Ile Phe Thr Glu Ile Gly Thr Ile Ala Ala Gly Ile Pro
945 950 955 960
Asp Leu Ala Leu Ser Ala Leu Leu Arg Gly Gln Ile Gln Gly Val Thr
965 970 975
Pro Leu Ala Ile Ser Val Ile Pro Pro Pro Lys Phe Ala Val Val Phe
980 985 990
Ser Pro Ile Gln Leu Ser Ser Leu Thr Ser Ala Gln Ala Val Ala Val
995 1000 1005
Thr Pro Glu Gln Met Ala Phe Leu Ser Pro Glu Gln Arg Arg Ala
1010 1015 1020
Val Ala Trp Ala Gln His Glu Gly Lys Glu Ser Pro Glu Gln Gln
1025 1030 1035
Gly Arg Ser Thr Ala Trp Gly Leu Gln Asp Trp Ser Arg Pro Ser
1040 1045 1050
Trp Ser Leu Val Leu Thr Ile Ser Phe Leu Gly His Leu Leu
1055 1060 1065
<210> 24
<211> 1063
<212> PRT
<213> Mus musculus
<400> 24
Cys Phe Ser Pro Val Leu Trp Asp Leu Leu Gln Arg Glu Lys Ser Val
1 5 10 15
Trp Ala Leu Arg Thr Leu Val Lys Ala Tyr Leu Arg Met Pro Pro Glu
20 25 30
Asp Leu Gln Gln Leu Val Leu Ser Ala Glu Met Glu Ala Ala Gln Gly
35 40 45
Phe Leu Thr Leu Met Leu Arg Ser Trp Ala Lys Leu Lys Val Gln Pro
50 55 60
Ser Glu Glu Gln Ala Met Gly Arg Leu Thr Ala Leu Leu Leu Gln Arg
65 70 75 80
Tyr Pro Arg Leu Thr Ser Gln Leu Phe Ile Asp Met Ser Pro Leu Ile
85 90 95
Pro Phe Leu Ala Val Pro Asp Leu Met Arg Phe Pro Pro Ser Leu Leu
100 105 110
Ala Asn Asp Ser Val Leu Ala Ala Ile Arg Asp His Ser Ser Gly Met
115 120 125
Lys Pro Glu Gln Lys Glu Ala Leu Ala Lys Arg Leu Leu Ala Pro Glu
130 135 140
Leu Phe Gly Glu Val Pro Asp Trp Pro Gln Glu Leu Leu Trp Ala Ala
145 150 155 160
Leu Pro Leu Leu Pro His Leu Pro Leu Glu Ser Phe Leu Gln Leu Ser
165 170 175
Pro His Gln Ile Gln Ala Leu Glu Asp Ser Trp Pro Val Ala Asp Leu
180 185 190
Gly Pro Gly His Ala Arg His Val Leu Arg Ser Leu Val Asn Gln Ser
195 200 205
Met Glu Asp Gly Glu Glu Gln Val Leu Arg Leu Gly Ser Leu Ala Cys
210 215 220
Phe Leu Ser Pro Glu Glu Leu Gln Ser Leu Val Pro Leu Ser Asp Pro
225 230 235 240
Met Gly Pro Val Glu Gln Gly Leu Leu Glu Cys Ala Ala Asn Gly Thr
245 250 255
Leu Ser Pro Glu Gly Arg Val Ala Tyr Glu Leu Leu Gly Val Leu Arg
260 265 270
Ser Ser Gly Gly Thr Val Leu Ser Pro Arg Glu Leu Arg Val Trp Ala
275 280 285
Pro Leu Phe Pro Gln Leu Gly Leu Arg Phe Leu Gln Glu Leu Ser Glu
290 295 300
Thr Gln Leu Arg Ala Met Leu Pro Ala Leu Gln Gly Ala Ser Val Thr
305 310 315 320
Pro Ala Gln Ala Val Leu Leu Phe Gly Arg Leu Leu Pro Lys His Asp
325 330 335
Leu Ser Leu Glu Glu Leu Cys Ser Leu His Pro Leu Leu Pro Gly Leu
340 345 350
Ser Pro Gln Thr Leu Gln Ala Ile Pro Lys Arg Val Leu Val Gly Ala
355 360 365
Cys Ser Cys Leu Gly Pro Glu Leu Ser Arg Leu Ser Ala Cys Gln Ile
370 375 380
Ala Ala Leu Leu Gln Thr Phe Arg Val Lys Asp Gly Val Lys Asn Met
385 390 395 400
Gly Ala Ala Gly Ala Gly Ser Ala Val Cys Ile Pro Gly Gln Pro Thr
405 410 415
Thr Trp Pro Asp Cys Leu Leu Pro Leu Leu Pro Leu Lys Leu Leu Gln
420 425 430
Leu Asp Ala Ala Ala Leu Leu Ala Asn Arg Arg Leu Tyr Arg Gln Leu
435 440 445
Pro Trp Ser Glu Gln Gln Ala Gln Phe Leu Trp Lys Lys Met Gln Val
450 455 460
Pro Thr Asn Leu Ser Leu Arg Asn Leu Gln Ala Leu Gly Asn Leu Ala
465 470 475 480
Gly Gly Met Thr Cys Glu Phe Leu Gln Gln Ile Ser Ser Met Val Asp
485 490 495
Phe Leu Asp Val Val His Met Leu Tyr Gln Leu Pro Thr Gly Val Arg
500 505 510
Glu Ser Leu Arg Ala Cys Ile Trp Thr Glu Leu Gln Arg Arg Met Thr
515 520 525
Met Pro Glu Pro Glu Leu Thr Thr Leu Gly Pro Glu Leu Ser Glu Leu
530 535 540
Asp Thr Lys Leu Leu Leu Asp Leu Pro Ile Gln Leu Met Asp Arg Leu
545 550 555 560
Ser Asn Asp Ser Ile Met Leu Val Val Glu Met Val Gln Gly Ala Pro
565 570 575
Glu Gln Leu Leu Ala Leu Thr Pro Leu His Gln Thr Ala Leu Ala Glu
580 585 590
Arg Ala Leu Lys Asn Leu Ala Pro Lys Glu Thr Pro Ile Ser Lys Glu
595 600 605
Val Leu Glu Thr Leu Gly Pro Leu Val Gly Phe Leu Gly Ile Glu Ser
610 615 620
Thr Arg Arg Ile Pro Leu Pro Ile Leu Leu Ser His Leu Ser Gln Leu
625 630 635 640
Gln Gly Phe Cys Leu Gly Glu Thr Phe Ala Thr Glu Leu Gly Trp Leu
645 650 655
Leu Leu Gln Glu Pro Val Leu Gly Lys Pro Glu Leu Trp Ser Gln Asp
660 665 670
Glu Ile Glu Gln Ala Gly Arg Leu Val Phe Thr Leu Ser Ala Glu Ala
675 680 685
Ile Ser Ser Ile Pro Arg Glu Ala Leu Gly Pro Glu Thr Leu Glu Arg
690 695 700
Leu Leu Gly Lys His Gln Ser Trp Glu Gln Ser Arg Val Gly His Leu
705 710 715 720
Cys Gly Glu Ser Gln Leu Ala His Lys Lys Ala Ala Leu Val Ala Gly
725 730 735
Ile Val His Pro Ala Ala Glu Gly Leu Gln Glu Pro Val Pro Asn Cys
740 745 750
Ala Asp Ile Arg Gly Thr Phe Pro Ala Ala Trp Ser Ala Thr Gln Ile
755 760 765
Ser Glu Met Glu Leu Ser Asp Phe Glu Asp Cys Leu Ser Leu Phe Ala
770 775 780
Gly Asp Pro Gly Leu Gly Pro Glu Glu Leu Arg Ala Ala Met Gly Lys
785 790 795 800
Ala Lys Gln Leu Trp Gly Pro Pro Arg Gly Phe Arg Pro Glu Gln Ile
805 810 815
Leu Gln Leu Gly Arg Leu Leu Ile Gly Leu Gly Glu Arg Glu Leu Gln
820 825 830
Glu Leu Thr Leu Val Asp Trp Gly Val Leu Ser Ser Leu Gly Gln Ile
835 840 845
Asp Gly Trp Ser Ser Met Gln Leu Arg Ala Val Val Ser Ser Phe Leu
850 855 860
Arg Gln Ser Gly Arg His Val Ser His Leu Asp Phe Ile Tyr Leu Thr
865 870 875 880
Ala Leu Gly Tyr Thr Val Cys Gly Leu Arg Pro Glu Glu Leu Gln His
885 890 895
Ile Ser Ser Trp Glu Phe Ser Gln Ala Ala Leu Phe Leu Gly Ser Leu
900 905 910
His Leu Pro Cys Ser Glu Glu Gln Leu Glu Val Leu Ala Tyr Leu Leu
915 920 925
Val Leu Pro Gly Gly Phe Gly Pro Val Ser Asn Trp Gly Pro Glu Ile
930 935 940
Phe Thr Glu Ile Gly Thr Ile Ala Ala Gly Ile Pro Asp Leu Ala Leu
945 950 955 960
Ser Ala Leu Leu Arg Gly Gln Ile Gln Gly Leu Thr Pro Leu Ala Ile
965 970 975
Ser Val Ile Pro Ala Pro Lys Phe Ala Val Val Phe Asn Pro Ile Gln
980 985 990
Leu Ser Ser Leu Thr Arg Gly Gln Ala Val Ala Val Thr Pro Glu Gln
995 1000 1005
Leu Ala Tyr Leu Ser Pro Glu Gln Arg Arg Ala Val Ala Trp Ala
1010 1015 1020
Gln His Glu Gly Lys Glu Ile Pro Glu Gln Leu Gly Arg Asn Ser
1025 1030 1035
Ala Trp Gly Leu Tyr Asp Trp Phe Gln Ala Ser Trp Ala Leu Ala
1040 1045 1050
Leu Pro Val Ser Ile Phe Gly His Leu Leu
1055 1060
<210> 25
<211> 1775
<212> PRT
<213> Homo sapiens
<400> 25
Met Ala Leu Ser Leu Trp Pro Leu Leu Leu Leu Leu Leu Leu Leu Leu
1 5 10 15
Leu Leu Ser Phe Ala Val Thr Leu Ala Pro Thr Gly Pro His Ser Leu
20 25 30
Asp Pro Gly Leu Ser Phe Leu Lys Ser Leu Leu Ser Thr Leu Asp Gln
35 40 45
Ala Pro Gln Gly Ser Leu Ser Arg Ser Arg Phe Phe Thr Phe Leu Ala
50 55 60
Asn Ile Ser Ser Ser Phe Glu Pro Gly Arg Met Gly Glu Gly Pro Val
65 70 75 80
Gly Glu Pro Pro Pro Leu Gln Pro Pro Ala Leu Arg Leu His Asp Phe
85 90 95
Leu Val Thr Leu Arg Gly Ser Pro Asp Trp Glu Pro Met Leu Gly Leu
100 105 110
Leu Gly Asp Met Leu Ala Leu Leu Gly Gln Glu Gln Thr Pro Arg Asp
115 120 125
Phe Leu Val His Gln Ala Gly Val Leu Gly Gly Leu Val Glu Val Leu
130 135 140
Leu Gly Ala Leu Val Pro Gly Gly Pro Pro Thr Pro Thr Arg Pro Pro
145 150 155 160
Cys Thr Arg Asp Gly Pro Ser Asp Cys Val Leu Ala Ala Asp Trp Leu
165 170 175
Pro Ser Leu Leu Leu Leu Leu Glu Gly Thr Arg Trp Gln Ala Leu Val
180 185 190
Gln Val Gln Pro Ser Val Asp Pro Thr Asn Ala Thr Gly Leu Asp Gly
195 200 205
Arg Glu Ala Ala Pro His Phe Leu Gln Gly Leu Leu Gly Leu Leu Thr
210 215 220
Pro Thr Gly Glu Leu Gly Ser Lys Glu Ala Leu Trp Gly Gly Leu Leu
225 230 235 240
Arg Thr Val Gly Ala Pro Leu Tyr Ala Ala Phe Gln Glu Gly Leu Leu
245 250 255
Arg Val Thr His Ser Leu Gln Asp Glu Val Phe Ser Ile Leu Gly Gln
260 265 270
Pro Glu Pro Asp Thr Asn Gly Gln Cys Gln Gly Gly Asn Leu Gln Gln
275 280 285
Leu Leu Leu Trp Gly Val Arg His Asn Leu Ser Trp Asp Val Gln Ala
290 295 300
Leu Gly Phe Leu Ser Gly Ser Pro Pro Pro Pro Pro Ala Leu Leu His
305 310 315 320
Cys Leu Ser Thr Gly Val Pro Leu Pro Arg Ala Ser Gln Pro Ser Ala
325 330 335
His Ile Ser Pro Arg Gln Arg Arg Ala Ile Thr Val Glu Ala Leu Cys
340 345 350
Glu Asn His Leu Gly Pro Ala Pro Pro Tyr Ser Ile Ser Asn Phe Ser
355 360 365
Ile His Leu Leu Cys Gln His Thr Lys Pro Ala Thr Pro Gln Pro His
370 375 380
Pro Ser Thr Thr Ala Ile Cys Gln Thr Ala Val Trp Tyr Ala Val Ser
385 390 395 400
Trp Ala Pro Gly Ala Gln Gly Trp Leu Gln Ala Cys His Asp Gln Phe
405 410 415
Pro Asp Glu Phe Leu Asp Ala Ile Cys Ser Asn Leu Ser Phe Ser Ala
420 425 430
Leu Ser Gly Ser Asn Arg Arg Leu Val Lys Arg Leu Cys Ala Gly Leu
435 440 445
Leu Pro Pro Pro Thr Ser Cys Pro Glu Gly Leu Pro Pro Val Pro Leu
450 455 460
Thr Pro Asp Ile Phe Trp Gly Cys Phe Leu Glu Asn Glu Thr Leu Trp
465 470 475 480
Ala Glu Arg Leu Cys Gly Glu Ala Ser Leu Gln Ala Val Pro Pro Ser
485 490 495
Asn Gln Ala Trp Val Gln His Val Cys Gln Gly Pro Thr Pro Asp Val
500 505 510
Thr Ala Ser Pro Pro Cys His Ile Gly Pro Cys Gly Glu Arg Cys Pro
515 520 525
Asp Gly Gly Ser Phe Leu Val Met Val Cys Ala Asn Asp Thr Met Tyr
530 535 540
Glu Val Leu Val Pro Phe Trp Pro Trp Leu Ala Gly Gln Cys Arg Ile
545 550 555 560
Ser Arg Gly Gly Asn Asp Thr Cys Phe Leu Glu Gly Leu Leu Gly Pro
565 570 575
Leu Leu Pro Ser Leu Pro Pro Leu Gly Pro Ser Pro Leu Cys Leu Thr
580 585 590
Pro Gly Pro Phe Leu Leu Gly Met Leu Ser Gln Leu Pro Arg Cys Gln
595 600 605
Ser Ser Val Pro Ala Leu Ala His Pro Thr Arg Leu His Tyr Leu Leu
610 615 620
Arg Leu Leu Thr Phe Leu Leu Gly Pro Gly Ala Gly Gly Ala Glu Ala
625 630 635 640
Gln Gly Met Leu Gly Arg Ala Leu Leu Leu Ser Ser Leu Pro Asp Asn
645 650 655
Cys Ser Phe Trp Asp Ala Phe Arg Pro Glu Gly Arg Arg Ser Val Leu
660 665 670
Arg Thr Ile Gly Glu Tyr Leu Glu Gln Asp Glu Glu Gln Pro Thr Pro
675 680 685
Ser Gly Phe Glu Pro Thr Val Asn Pro Ser Ser Gly Ile Ser Lys Met
690 695 700
Glu Leu Leu Ala Cys Phe Ser Pro Val Leu Trp Asp Leu Leu Gln Arg
705 710 715 720
Glu Lys Ser Val Trp Ala Leu Gln Ile Leu Val Gln Ala Tyr Leu His
725 730 735
Met Pro Pro Glu Asn Leu Gln Gln Leu Val Leu Ser Ala Glu Arg Glu
740 745 750
Ala Ala Gln Gly Phe Leu Thr Leu Met Leu Gln Gly Lys Leu Gln Gly
755 760 765
Lys Leu Gln Val Pro Pro Ser Glu Glu Gln Ala Leu Gly Arg Leu Thr
770 775 780
Ala Leu Leu Leu Gln Arg Tyr Pro Arg Leu Thr Ser Gln Leu Phe Ile
785 790 795 800
Asp Leu Ser Pro Leu Ile Pro Phe Leu Ala Val Ser Asp Leu Met Arg
805 810 815
Phe Pro Pro Ser Leu Leu Ala Asn Asp Ser Val Leu Ala Ala Ile Arg
820 825 830
Asp Tyr Ser Pro Gly Met Arg Pro Glu Gln Lys Glu Ala Leu Ala Lys
835 840 845
Arg Leu Leu Ala Pro Glu Leu Phe Gly Glu Val Pro Ala Trp Pro Gln
850 855 860
Glu Leu Leu Trp Ala Val Leu Pro Leu Leu Pro His Leu Pro Leu Glu
865 870 875 880
Asn Phe Leu Gln Leu Ser Pro His Gln Ile Gln Ala Leu Glu Asp Ser
885 890 895
Trp Pro Ala Ala Gly Leu Gly Pro Gly His Ala Arg His Val Leu Arg
900 905 910
Ser Leu Val Asn Gln Ser Val Gln Asp Gly Glu Glu Gln Val Arg Arg
915 920 925
Leu Gly Pro Leu Ala Cys Phe Leu Ser Pro Glu Glu Leu Gln Ser Leu
930 935 940
Val Pro Leu Ser Asp Pro Thr Gly Pro Val Glu Arg Gly Leu Leu Glu
945 950 955 960
Cys Ala Ala Asn Gly Thr Leu Ser Pro Glu Gly Arg Val Ala Tyr Glu
965 970 975
Leu Leu Gly Val Leu Arg Ser Ser Gly Gly Ala Val Leu Ser Pro Arg
980 985 990
Glu Leu Arg Val Trp Ala Pro Leu Phe Ser Gln Leu Gly Leu Arg Phe
995 1000 1005
Leu Gln Glu Leu Ser Glu Pro Gln Leu Arg Ala Met Leu Pro Val
1010 1015 1020
Leu Gln Gly Thr Ser Val Thr Pro Ala Gln Ala Val Leu Leu Leu
1025 1030 1035
Gly Arg Leu Leu Pro Arg His Asp Leu Ser Leu Glu Glu Leu Cys
1040 1045 1050
Ser Leu His Leu Leu Leu Pro Gly Leu Ser Pro Gln Thr Leu Gln
1055 1060 1065
Ala Ile Pro Arg Arg Val Leu Val Gly Ala Cys Ser Cys Leu Ala
1070 1075 1080
Pro Glu Leu Ser Arg Leu Ser Ala Cys Gln Thr Ala Ala Leu Leu
1085 1090 1095
Gln Thr Phe Arg Val Lys Asp Gly Val Lys Asn Met Gly Thr Thr
1100 1105 1110
Gly Ala Gly Pro Ala Val Cys Ile Pro Gly Gln Pro Ile Pro Thr
1115 1120 1125
Thr Trp Pro Asp Cys Leu Leu Pro Leu Leu Pro Leu Lys Leu Leu
1130 1135 1140
Gln Leu Asp Ser Leu Ala Leu Leu Ala Asn Arg Arg Arg Tyr Trp
1145 1150 1155
Glu Leu Pro Trp Ser Glu Gln Gln Ala Gln Phe Leu Trp Lys Lys
1160 1165 1170
Met Gln Val Pro Thr Asn Leu Thr Leu Arg Asn Leu Gln Ala Leu
1175 1180 1185
Gly Thr Leu Ala Gly Gly Met Ser Cys Glu Phe Leu Gln Gln Ile
1190 1195 1200
Asn Ser Met Val Asp Phe Leu Glu Val Val His Met Ile Tyr Gln
1205 1210 1215
Leu Pro Thr Arg Val Arg Gly Ser Leu Arg Ala Cys Ile Trp Ala
1220 1225 1230
Glu Leu Gln Arg Arg Met Ala Met Pro Glu Pro Glu Trp Thr Thr
1235 1240 1245
Val Gly Pro Glu Leu Asn Gly Leu Asp Ser Lys Leu Leu Leu Asp
1250 1255 1260
Leu Pro Ile Gln Leu Met Asp Arg Leu Ser Asn Glu Ser Ile Met
1265 1270 1275
Leu Val Val Glu Leu Val Gln Arg Ala Pro Glu Gln Leu Leu Ala
1280 1285 1290
Leu Thr Pro Leu His Gln Ala Ala Leu Ala Glu Arg Ala Leu Gln
1295 1300 1305
Asn Leu Ala Pro Lys Glu Thr Pro Val Ser Gly Glu Val Leu Glu
1310 1315 1320
Thr Leu Gly Pro Leu Val Gly Phe Leu Gly Thr Glu Ser Thr Arg
1325 1330 1335
Gln Ile Pro Leu Gln Ile Leu Leu Ser His Leu Ser Gln Leu Gln
1340 1345 1350
Gly Phe Cys Leu Gly Glu Thr Phe Ala Thr Glu Leu Gly Trp Leu
1355 1360 1365
Leu Leu Gln Glu Ser Val Leu Gly Lys Pro Glu Leu Trp Ser Gln
1370 1375 1380
Asp Glu Val Glu Gln Ala Gly Arg Leu Val Phe Thr Leu Ser Thr
1385 1390 1395
Glu Ala Ile Ser Leu Ile Pro Arg Glu Ala Leu Gly Pro Glu Thr
1400 1405 1410
Leu Glu Arg Leu Leu Glu Lys Gln Gln Ser Trp Glu Gln Ser Arg
1415 1420 1425
Val Gly Gln Leu Cys Arg Glu Pro Gln Leu Ala Ala Lys Lys Ala
1430 1435 1440
Ala Leu Val Ala Gly Val Val Arg Pro Ala Ala Glu Asp Leu Pro
1445 1450 1455
Glu Pro Val Pro Asn Cys Ala Asp Val Arg Gly Thr Phe Pro Ala
1460 1465 1470
Ala Trp Ser Ala Thr Gln Ile Ala Glu Met Glu Leu Ser Asp Phe
1475 1480 1485
Glu Asp Cys Leu Thr Leu Phe Ala Gly Asp Pro Gly Leu Gly Pro
1490 1495 1500
Glu Glu Leu Arg Ala Ala Met Gly Lys Ala Lys Gln Leu Trp Gly
1505 1510 1515
Pro Pro Arg Gly Phe Arg Pro Glu Gln Ile Leu Gln Leu Gly Arg
1520 1525 1530
Leu Leu Ile Gly Leu Gly Asp Arg Glu Leu Gln Glu Leu Ile Leu
1535 1540 1545
Val Asp Trp Gly Val Leu Ser Thr Leu Gly Gln Ile Asp Gly Trp
1550 1555 1560
Ser Thr Thr Gln Leu Arg Ile Val Val Ser Ser Phe Leu Arg Gln
1565 1570 1575
Ser Gly Arg His Val Ser His Leu Asp Phe Val His Leu Thr Ala
1580 1585 1590
Leu Gly Tyr Thr Leu Cys Gly Leu Arg Pro Glu Glu Leu Gln His
1595 1600 1605
Ile Ser Ser Trp Glu Phe Ser Gln Ala Ala Leu Phe Leu Gly Thr
1610 1615 1620
Leu His Leu Gln Cys Ser Glu Glu Gln Leu Glu Val Leu Ala His
1625 1630 1635
Leu Leu Val Leu Pro Gly Gly Phe Gly Pro Ile Ser Asn Trp Gly
1640 1645 1650
Pro Glu Ile Phe Thr Glu Ile Gly Thr Ile Ala Ala Gly Ile Pro
1655 1660 1665
Asp Leu Ala Leu Ser Ala Leu Leu Arg Gly Gln Ile Gln Gly Val
1670 1675 1680
Thr Pro Leu Ala Ile Ser Val Ile Pro Pro Pro Lys Phe Ala Val
1685 1690 1695
Val Phe Ser Pro Ile Gln Leu Ser Ser Leu Thr Ser Ala Gln Ala
1700 1705 1710
Val Ala Val Thr Pro Glu Gln Met Ala Phe Leu Ser Pro Glu Gln
1715 1720 1725
Arg Arg Ala Val Ala Trp Ala Gln His Glu Gly Lys Glu Ser Pro
1730 1735 1740
Glu Gln Gln Gly Arg Ser Thr Ala Trp Gly Leu Gln Asp Trp Ser
1745 1750 1755
Arg Pro Ser Trp Ser Leu Val Leu Thr Ile Ser Phe Leu Gly His
1760 1765 1770
Leu Leu
1775
<210> 26
<211> 1809
<212> PRT
<213> Mus musculus
<400> 26
Met Ala Leu Ser Leu Gln Pro Gln Leu Leu Leu Leu Leu Ser Leu Leu
1 5 10 15
Pro Gln Glu Val Thr Ser Ala Pro Thr Gly Pro Gln Ser Leu Asp Ala
20 25 30
Gly Leu Ser Leu Leu Lys Ser Phe Val Ala Thr Leu Asp Gln Ala Pro
35 40 45
Gln Arg Ser Leu Ser Gln Ser Arg Phe Ser Ala Phe Leu Ala Asn Ile
50 55 60
Ser Ser Ser Phe Gln Leu Gly Arg Met Gly Glu Gly Pro Val Gly Glu
65 70 75 80
Pro Pro Pro Leu Gln Pro Pro Ala Leu Arg Leu His Asp Phe Leu Val
85 90 95
Thr Leu Arg Gly Ser Pro Asp Trp Glu Pro Met Leu Gly Leu Leu Gly
100 105 110
Asp Val Leu Ala Leu Leu Gly Gln Glu Gln Thr Pro Arg Asp Phe Leu
115 120 125
Val His Gln Ala Gly Val Leu Gly Gly Leu Val Glu Ala Leu Leu Gly
130 135 140
Ala Leu Val Pro Gly Gly Pro Pro Ala Pro Thr Arg Pro Pro Cys Thr
145 150 155 160
Arg Asp Gly Pro Ser Asp Cys Val Leu Ala Ala Asp Trp Leu Pro Ser
165 170 175
Leu Met Leu Leu Leu Glu Gly Thr Arg Trp Gln Ala Leu Val Gln Leu
180 185 190
Gln Pro Ser Val Asp Pro Thr Asn Ala Thr Gly Leu Asp Gly Arg Glu
195 200 205
Pro Ala Pro His Phe Leu Gln Gly Leu Leu Gly Leu Leu Thr Pro Ala
210 215 220
Gly Glu Leu Gly Ser Glu Glu Ala Leu Trp Gly Gly Leu Leu Arg Thr
225 230 235 240
Val Gly Ala Pro Leu Tyr Ala Ala Phe Gln Glu Gly Leu Leu Arg Val
245 250 255
Thr His Ser Leu Gln Asp Glu Val Phe Ser Ile Met Gly Gln Pro Glu
260 265 270
Pro Asp Ala Ser Gly Gln Cys Gln Gly Gly Asn Leu Gln Gln Leu Leu
275 280 285
Leu Trp Gly Met Arg Asn Asn Leu Ser Trp Asp Ala Arg Ala Leu Gly
290 295 300
Phe Leu Ser Gly Ser Pro Pro Pro Pro Pro Ala Leu Leu His Cys Leu
305 310 315 320
Ser Arg Gly Val Pro Leu Pro Arg Ala Ser Gln Pro Ala Ala His Ile
325 330 335
Ser Pro Arg Gln Arg Arg Ala Ile Ser Val Glu Ala Leu Cys Glu Asn
340 345 350
His Ser Gly Pro Glu Pro Pro Tyr Ser Ile Ser Asn Phe Ser Ile Tyr
355 360 365
Leu Leu Cys Gln His Ile Lys Pro Ala Thr Pro Arg Pro Pro Pro Thr
370 375 380
Thr Pro Arg Pro Pro Pro Thr Thr Pro Gln Pro Pro Pro Thr Thr Thr
385 390 395 400
Gln Pro Ile Pro Asp Thr Thr Gln Pro Pro Pro Val Thr Pro Arg Pro
405 410 415
Pro Pro Thr Thr Pro Gln Pro Pro Pro Ser Thr Ala Val Ile Cys Gln
420 425 430
Thr Ala Val Trp Tyr Ala Val Ser Trp Ala Pro Gly Ala Arg Gly Trp
435 440 445
Leu Gln Ala Cys His Asp Gln Phe Pro Asp Gln Phe Leu Asp Met Ile
450 455 460
Cys Gly Asn Leu Ser Phe Ser Ala Leu Ser Gly Pro Ser Arg Pro Leu
465 470 475 480
Val Lys Gln Leu Cys Ala Gly Leu Leu Pro Pro Pro Thr Ser Cys Pro
485 490 495
Pro Gly Leu Ile Pro Val Pro Leu Thr Pro Glu Ile Phe Trp Gly Cys
500 505 510
Phe Leu Glu Asn Glu Thr Leu Trp Ala Glu Arg Leu Cys Val Glu Asp
515 520 525
Ser Leu Gln Ala Val Pro Pro Arg Asn Gln Ala Trp Val Gln His Val
530 535 540
Cys Arg Gly Pro Thr Leu Asp Ala Thr Asp Phe Pro Pro Cys Arg Val
545 550 555 560
Gly Pro Cys Gly Glu Arg Cys Pro Asp Gly Gly Ser Phe Leu Leu Met
565 570 575
Val Cys Ala Asn Asp Thr Leu Tyr Glu Ala Leu Val Pro Phe Trp Ala
580 585 590
Trp Leu Ala Gly Gln Cys Arg Ile Ser Arg Gly Gly Asn Asp Thr Cys
595 600 605
Phe Leu Glu Gly Met Leu Gly Pro Leu Leu Pro Ser Leu Pro Pro Leu
610 615 620
Gly Pro Ser Pro Leu Cys Leu Ala Pro Gly Pro Phe Leu Leu Gly Met
625 630 635 640
Leu Ser Gln Leu Pro Arg Cys Gln Ser Ser Val Pro Ala Leu Ala His
645 650 655
Pro Thr Arg Leu His Tyr Leu Leu Arg Leu Leu Thr Phe Leu Leu Gly
660 665 670
Pro Gly Thr Gly Gly Ala Glu Thr Gln Gly Met Leu Gly Gln Ala Leu
675 680 685
Leu Leu Ser Ser Leu Pro Asp Asn Cys Ser Phe Trp Asp Ala Phe Arg
690 695 700
Pro Glu Gly Arg Arg Ser Val Leu Arg Thr Val Gly Glu Tyr Leu Gln
705 710 715 720
Arg Glu Glu Pro Thr Pro Pro Gly Leu Asp Ser Ser Leu Ser Leu Gly
725 730 735
Ser Gly Met Ser Lys Met Glu Leu Leu Ser Cys Phe Ser Pro Val Leu
740 745 750
Trp Asp Leu Leu Gln Arg Glu Lys Ser Val Trp Ala Leu Arg Thr Leu
755 760 765
Val Lys Ala Tyr Leu Arg Met Pro Pro Glu Asp Leu Gln Gln Leu Val
770 775 780
Leu Ser Ala Glu Met Glu Ala Ala Gln Gly Phe Leu Thr Leu Met Leu
785 790 795 800
Arg Ser Trp Ala Lys Leu Lys Val Gln Pro Ser Glu Glu Gln Ala Met
805 810 815
Gly Arg Leu Thr Ala Leu Leu Leu Gln Arg Tyr Pro Arg Leu Thr Ser
820 825 830
Gln Leu Phe Ile Asp Met Ser Pro Leu Ile Pro Phe Leu Ala Val Pro
835 840 845
Asp Leu Met Arg Phe Pro Pro Ser Leu Leu Ala Asn Asp Ser Val Leu
850 855 860
Ala Ala Ile Arg Asp His Ser Ser Gly Met Lys Pro Glu Gln Lys Glu
865 870 875 880
Ala Leu Ala Lys Arg Leu Leu Ala Pro Glu Leu Phe Gly Glu Val Pro
885 890 895
Asp Trp Pro Gln Glu Leu Leu Trp Ala Ala Leu Pro Leu Leu Pro His
900 905 910
Leu Pro Leu Glu Ser Phe Leu Gln Leu Ser Pro His Gln Ile Gln Ala
915 920 925
Leu Glu Asp Ser Trp Pro Val Ala Asp Leu Gly Pro Gly His Ala Arg
930 935 940
His Val Leu Arg Ser Leu Val Asn Gln Ser Met Glu Asp Gly Glu Glu
945 950 955 960
Gln Val Leu Arg Leu Gly Ser Leu Ala Cys Phe Leu Ser Pro Glu Glu
965 970 975
Leu Gln Ser Leu Val Pro Leu Ser Asp Pro Met Gly Pro Val Glu Gln
980 985 990
Gly Leu Leu Glu Cys Ala Ala Asn Gly Thr Leu Ser Pro Glu Gly Arg
995 1000 1005
Val Ala Tyr Glu Leu Leu Gly Val Leu Arg Ser Ser Gly Gly Thr
1010 1015 1020
Val Leu Ser Pro Arg Glu Leu Arg Val Trp Ala Pro Leu Phe Pro
1025 1030 1035
Gln Leu Gly Leu Arg Phe Leu Gln Glu Leu Ser Glu Thr Gln Leu
1040 1045 1050
Arg Ala Met Leu Pro Ala Leu Gln Gly Ala Ser Val Thr Pro Ala
1055 1060 1065
Gln Ala Val Leu Leu Phe Gly Arg Leu Leu Pro Lys His Asp Leu
1070 1075 1080
Ser Leu Glu Glu Leu Cys Ser Leu His Pro Leu Leu Pro Gly Leu
1085 1090 1095
Ser Pro Gln Thr Leu Gln Ala Ile Pro Lys Arg Val Leu Val Gly
1100 1105 1110
Ala Cys Ser Cys Leu Gly Pro Glu Leu Ser Arg Leu Ser Ala Cys
1115 1120 1125
Gln Ile Ala Ala Leu Leu Gln Thr Phe Arg Val Lys Asp Gly Val
1130 1135 1140
Lys Asn Met Gly Ala Ala Gly Ala Gly Ser Ala Val Cys Ile Pro
1145 1150 1155
Gly Gln Pro Thr Thr Trp Pro Asp Cys Leu Leu Pro Leu Leu Pro
1160 1165 1170
Leu Lys Leu Leu Gln Leu Asp Ala Ala Ala Leu Leu Ala Asn Arg
1175 1180 1185
Arg Leu Tyr Arg Gln Leu Pro Trp Ser Glu Gln Gln Ala Gln Phe
1190 1195 1200
Leu Trp Lys Lys Met Gln Val Pro Thr Asn Leu Ser Leu Arg Asn
1205 1210 1215
Leu Gln Ala Leu Gly Asn Leu Ala Gly Gly Met Thr Cys Glu Phe
1220 1225 1230
Leu Gln Gln Ile Ser Ser Met Val Asp Phe Leu Asp Val Val His
1235 1240 1245
Met Leu Tyr Gln Leu Pro Thr Gly Val Arg Glu Ser Leu Arg Ala
1250 1255 1260
Cys Ile Trp Thr Glu Leu Gln Arg Arg Met Thr Met Pro Glu Pro
1265 1270 1275
Glu Leu Thr Thr Leu Gly Pro Glu Leu Ser Glu Leu Asp Thr Lys
1280 1285 1290
Leu Leu Leu Asp Leu Pro Ile Gln Leu Met Asp Arg Leu Ser Asn
1295 1300 1305
Asp Ser Ile Met Leu Val Val Glu Met Val Gln Gly Ala Pro Glu
1310 1315 1320
Gln Leu Leu Ala Leu Thr Pro Leu His Gln Thr Ala Leu Ala Glu
1325 1330 1335
Arg Ala Leu Lys Asn Leu Ala Pro Lys Glu Thr Pro Ile Ser Lys
1340 1345 1350
Glu Val Leu Glu Thr Leu Gly Pro Leu Val Gly Phe Leu Gly Ile
1355 1360 1365
Glu Ser Thr Arg Arg Ile Pro Leu Pro Ile Leu Leu Ser His Leu
1370 1375 1380
Ser Gln Leu Gln Gly Phe Cys Leu Gly Glu Thr Phe Ala Thr Glu
1385 1390 1395
Leu Gly Trp Leu Leu Leu Gln Glu Pro Val Leu Gly Lys Pro Glu
1400 1405 1410
Leu Trp Ser Gln Asp Glu Ile Glu Gln Ala Gly Arg Leu Val Phe
1415 1420 1425
Thr Leu Ser Ala Glu Ala Ile Ser Ser Ile Pro Arg Glu Ala Leu
1430 1435 1440
Gly Pro Glu Thr Leu Glu Arg Leu Leu Gly Lys His Gln Ser Trp
1445 1450 1455
Glu Gln Ser Arg Val Gly His Leu Cys Gly Glu Ser Gln Leu Ala
1460 1465 1470
His Lys Lys Ala Ala Leu Val Ala Gly Ile Val His Pro Ala Ala
1475 1480 1485
Glu Gly Leu Gln Glu Pro Val Pro Asn Cys Ala Asp Ile Arg Gly
1490 1495 1500
Thr Phe Pro Ala Ala Trp Ser Ala Thr Gln Ile Ser Glu Met Glu
1505 1510 1515
Leu Ser Asp Phe Glu Asp Cys Leu Ser Leu Phe Ala Gly Asp Pro
1520 1525 1530
Gly Leu Gly Pro Glu Glu Leu Arg Ala Ala Met Gly Lys Ala Lys
1535 1540 1545
Gln Leu Trp Gly Pro Pro Arg Gly Phe Arg Pro Glu Gln Ile Leu
1550 1555 1560
Gln Leu Gly Arg Leu Leu Ile Gly Leu Gly Glu Arg Glu Leu Gln
1565 1570 1575
Glu Leu Thr Leu Val Asp Trp Gly Val Leu Ser Ser Leu Gly Gln
1580 1585 1590
Ile Asp Gly Trp Ser Ser Met Gln Leu Arg Ala Val Val Ser Ser
1595 1600 1605
Phe Leu Arg Gln Ser Gly Arg His Val Ser His Leu Asp Phe Ile
1610 1615 1620
Tyr Leu Thr Ala Leu Gly Tyr Thr Val Cys Gly Leu Arg Pro Glu
1625 1630 1635
Glu Leu Gln His Ile Ser Ser Trp Glu Phe Ser Gln Ala Ala Leu
1640 1645 1650
Phe Leu Gly Ser Leu His Leu Pro Cys Ser Glu Glu Gln Leu Glu
1655 1660 1665
Val Leu Ala Tyr Leu Leu Val Leu Pro Gly Gly Phe Gly Pro Val
1670 1675 1680
Ser Asn Trp Gly Pro Glu Ile Phe Thr Glu Ile Gly Thr Ile Ala
1685 1690 1695
Ala Gly Ile Pro Asp Leu Ala Leu Ser Ala Leu Leu Arg Gly Gln
1700 1705 1710
Ile Gln Gly Leu Thr Pro Leu Ala Ile Ser Val Ile Pro Ala Pro
1715 1720 1725
Lys Phe Ala Val Val Phe Asn Pro Ile Gln Leu Ser Ser Leu Thr
1730 1735 1740
Arg Gly Gln Ala Val Ala Val Thr Pro Glu Gln Leu Ala Tyr Leu
1745 1750 1755
Ser Pro Glu Gln Arg Arg Ala Val Ala Trp Ala Gln His Glu Gly
1760 1765 1770
Lys Glu Ile Pro Glu Gln Leu Gly Arg Asn Ser Ala Trp Gly Leu
1775 1780 1785
Tyr Asp Trp Phe Gln Ala Ser Trp Ala Leu Ala Leu Pro Val Ser
1790 1795 1800
Ile Phe Gly His Leu Leu
1805
<210> 27
<211> 10
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 27
Glu Gln Lys Leu Ile Ser Glu Glu Asp Leu
1 5 10
<210> 28
<211> 8543
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 28
ccaatgatac gcgtcggtgc gggcctcttc gctattacgc cagctggcga aagggggatg 60
tgctgcaagg cgattaagtt gggtaacgcc agggttttcc cagtcacgac gttgtaaaac 120
gacggccagt gagcgcgcgt aatacgactc actatagggc gaattgggta catcgacggt 180
atcgggggag ctcgcagggt ctccattttg aagcgggagg tttgaacgcg cagccgccat 240
gccggggttt tacgagattg tgattaaggt ccccagcgac cttgacgagc atctgcccgg 300
catttctgac agctttgtga actgggtggc cgagaaggaa tgggagttgc cgccagattc 360
tgacatggat ctgaatctga ttgagcaggc acccctgacc gtggccgaga agctgcagcg 420
cgactttctg acggaatggc gccgtgtgag taaggccccg gaggctcttt tctttgtgca 480
atttgagaag ggagagagct acttccacat gcacgtgctc gtggaaacca ccggggtgaa 540
atccatggtt ttgggacgtt tcctgagtca gattcgcgaa aaactgattc agagaattta 600
ccgcgggatc gagccgactt tgccaaactg gttcgcggtc acaaagacca gaaatggcgc 660
cggaggcggg aacaaggtgg tggatgagtg ctacatcccc aattacttgc tccccaaaac 720
ccagcctgag ctccagtggg cgtggactaa tatggaacag tatttaagcg cctgtttgaa 780
tctcacggag cgtaaacggt tggtggcgca gcatctgacg cacgtgtcgc agacgcagga 840
gcagaacaaa gagaatcaga atcccaattc tgatgcgccg gtgatcagat caaaaacttc 900
agccaggtac atggagctgg tcgggtggct cgtggacaag gggattacct cggagaagca 960
gtggatccag gaggaccagg cctcatacat ctccttcaat gcggcctcca actcgcggtc 1020
ccaaatcaag gctgccttgg acaatgcggg aaagattatg agcctgacta aaaccgcccc 1080
cgactacctg gtgggccagc agcccgtgga ggacatttcc agcaatcgga tttataaaat 1140
tttggaacta aacgggtacg atccccaata tgcggcttcc gtctttctgg gatgggccac 1200
gaaaaagttc ggcaagagga acaccatctg gctgtttggg cctgcaacta ccgggaagac 1260
caacatcgcg gaggccatag cccacactgt gcccttctac gggtgcgtaa actggaccaa 1320
tgagaacttt cccttcaacg actgtgtgga caagatggtg atctggtggg aggaggggaa 1380
gatgaccgcc aaggtcgtgg agtcggccaa agccattctc ggaggaagca aggtgcgcgt 1440
ggaccagaaa tgcaagtcct cggcccagat agacccgact cccgtgatcg tcacctccaa 1500
caccaatatg tgcgccgtga ttgacgggaa ctcaacgacc ttcgaacacc agcagccgtt 1560
gcaagaccgg atgttcaaat ttgaactcac ccgccgtctg gatcatgact ttgggaaggt 1620
caccaagcag gaagtcaaag actttttccg gtgggcaaag gatcacgtgg ttgaggtgga 1680
gcatgaattc tacgtcaaaa agggtggagc caagaaaaga cccgccccca gtgacgcaga 1740
tataagtgag cccaaacggg tgcgcgagtc agttgcgcag ccatcgacgt cagacgcgga 1800
agcttcgatc aactacgcgg acaggtacca aaacaaatgt tctcgtcacg tgggcatgaa 1860
tctgatgctg tttccctgca gacaatgcga gagactgaat cagaattcaa atatctgctt 1920
cactcacggt gtcaaagact gtttagagtg ctttcccgtg tcagaatctc aacccgtttc 1980
tgtcgtcaaa aaggcgtatc agaaactgtg ctacattcat cacatcatgg gaaaggtgcc 2040
agacgcttgc actgcttgcg acctggtcaa tgtggacttg gatgactgtg tttctgaaca 2100
ataaatgact taaaccaggt atgagtcggc tggataaatc taaagtcata aacggcgctc 2160
tggaattact caatgaagtc ggtatcgaag gcctgacgac aaggaaactc gctcaaaagc 2220
tgggagttga gcagcctacc ctgtactggc acgtgaagaa caagcgggcc ctgctcgatg 2280
ccctggccat cgagatgctg gacaggcatc atacccactt ctgccccctg gaaggcgagt 2340
catggcaaga ctttctgcgg aacaacgcca agtcattccg ctgtgctctc ctctcacatc 2400
gcgacggggc taaagtgcat ctcggcaccc gcccaacaga gaaacagtac gaaaccctgg 2460
aaaatcagct cgcgttcctg tgtcagcaag gcttctccct ggagaacgca ctgtacgctc 2520
tgtccgccgt gggccacttt acactgggct gcgtattgga ggaacaggag catcaagtag 2580
caaaagagga aagagagaca cctaccaccg attctatgcc cccacttctg agacaagcaa 2640
ttgagctgtt cgaccggcag ggagccgaac ctgccttcct tttcggcctg gaactaatca 2700
tatgtggcct ggagaaacag ctaaagtgcg aaagcggcgg gccggccgac gcccttgacg 2760
attttgactt agacatgctc ccagccgatg cccttgacga ctttgacctt gatatgctgc 2820
ctgctgacgc tcttgacgat tttgaccttg acatgctccc cgggtaaatg catgaattcg 2880
atctagaggg ccctattcta tagtgtcacc taaatgctag agctcgctga tcagcctcga 2940
ctgtgccttc tagttgccag ccatctgttg tttgcccctc ccccgtgcct tccttgaccc 3000
tggaaggtgc cactcccact gtcctttcct aataaaatga ggaaattgca tcgcattgtc 3060
tgagtaggtg tcattctatt ctggggggtg gggtggggca ggacagcaag ggggaggatt 3120
gggaagacaa tagcaggcat gctggggatg cggtgggctc tatggcttct gaggcggaaa 3180
gaaccagctg gggctcgaat caagctatca agtgccacct gacgtctccc tatcagtgat 3240
agagaagtcg acacgtctcg agctccctat cagtgataga gaaggtacgt ctagaacgtc 3300
tccctatcag tgatagagaa gtcgacacgt ctcgagctcc ctatcagtga tagagaaggt 3360
acgtctagaa cgtctcccta tcagtgatag agaagtcgac acgtctcgag ctccctatca 3420
gtgatagaga aggtacgtct agaacgtctc cctatcagtg atagagaagt cgacacgtct 3480
cgagctccct atcagtgata gagaaggtac cccctatata agcagagaga tctgttcaaa 3540
tttgaactga ctaagcggct cccgccagat tttggcaaga ttactaagca ggaagtcaag 3600
gacttttttg cttgggcaaa ggtcaatcag gtgccggtga ctcacgagtt taaagttccc 3660
agggaattgg cgggaactaa aggggcggag aaatctctaa aacgcccact gggtgacgtc 3720
accaatacta gctataaaag tctggagaag cgggccaggc tctcatttgt tcccgagacg 3780
cctcgcagtt cagacgtgac tgttgatccc gctcctctgc gaccgctagc ttcgatcaac 3840
tacgcagaca ggtaccaaaa caagtgttct cgtcacgtgg gcattaatct gattctgttt 3900
ccctgcagac aatgcgagag aatgaatcag aactcaaata tctgcttcac tcacggacag 3960
aaagactgtt tagagtgctt tcccgtgtca gaatctcaac ccgtttctgt cgtcaaaaag 4020
gcgtatcaga aactgtgcta cattcatcat atcatgggaa aggtgccaga cgcttgcact 4080
gcctgcgatc tggtcaatgt ggatttggat gactgcatct ttgaacaata aatgacttaa 4140
gccaggtatg gctgccgatg gttatcttcc agattggctc gaggacaacc ttagtgaagg 4200
aattcgcgag tggtgggctt tgaaacctgg agcccctcaa cccaaggcaa atcaacaaca 4260
tcaagacaac gctagaggtc ttgtgcttcc gggttacaaa taccttggac ccggcaacgg 4320
actcgacaag ggggagccgg tcaacgcagc agacgcggcg gccctcgagc acgacaaagc 4380
ctacgaccag cagctcaagg ccggagacaa cccgtacctc aagtacaacc acgccgacgc 4440
cgagttccag gagcggctca aagaagatac gtcttttggg ggcaacctcg ggcgagcagt 4500
cttccaggcc aaaaagaggc ttcttgaacc tcttggtctg gttgaggaag cggctaagac 4560
ggctcctgga aagaagaggc ctgtagagca gtctcctcag gaaccggact cctccgcggg 4620
tattggcaaa tcgggtgcac agcccgctaa aaagagactc aatttcggtc agactggcga 4680
cacagagtca gtcccagacc ctcaaccaat cggagaacct cccgcagccc cctcaggtgt 4740
gggatctctt acaatggctt caggtggtgg cgcaccagtg gcagacaata acgaaggtgc 4800
cgatggagtg ggtagttcct cgggaaattg gcattgcgat tcccaatggc tgggggacag 4860
agtcatcacc accagcaccc gaacctgggc cctgcccacc tacaacaatc acctctacaa 4920
gcaaatctcc aacagcacat ctggaggatc ttcaaatgac aacgcctact tcggctacag 4980
caccccctgg gggtattttg acttcaacag attccactgc cacttctcac cacgtgactg 5040
gcagcgactc atcaacaaca actggggatt ccggcctaag cgactcaact tcaagctctt 5100
taacattcag gtcaaagagg ttacggacaa caatggagtc aagaccatcg ccaataacct 5160
taccagcacg gtccaggtct tcacggactc agactatcag ctcccgtacg tgctcgggtc 5220
ggctcacgag ggctgcctcc cgccgttccc agcggacgtt ttcatgattc ctcagtacgg 5280
gtatctgacg cttaatgatg gaagccaggc cgtgggtcgt tcgtcctttt actgcctgga 5340
atatttcccg tcgcaaatgc taagaacggg taacaacttc cagttcagct acgagtttga 5400
gaacgtacct ttccatagca gctacgctca cagccaaagc ctggaccgac taatgaatcc 5460
actcatcgac caatacttgt actatctctc tagaactatt aacggttctg gacagaatca 5520
acaaacgcta aaattcagtg tggccggacc cagcaacatg gctgtccagg gaagaaacta 5580
catacctgga cccagctacc gacaacaacg tgtctcaacc actgtgactc aaaacaacaa 5640
cagcgaattt gcttggcctg gagcttcttc ttgggctctc aatggacgta atagcttgat 5700
gaatcctgga cctgctatgg cctctcacaa agaaggagag gaccgtttct ttcctttgtc 5760
tggatcttta atttttggca aacaaggtac tggcagagac aacgtggatg cggacaaagt 5820
catgataacc aacgaagaag aaattaaaac tactaacccg gtagcaacgg agtcctatgg 5880
acaagtggcc acaaaccacc agagtgccca aactttggcg gtgcctttta aggcacaggc 5940
gcagaccggt tgggttcaaa accaaggaat acttccgggt atggtttggc aggacagaga 6000
tgtgtacctg caaggaccca tttgggccaa aattcctcac acggacggca actttcaccc 6060
ttctccgctg atgggagggt ttggaatgaa gcacccgcct cctcagatcc tcatcaaaaa 6120
cacacctgta cctgcggatc ctccaacggc cttcaacaag gacaagctga actctttcat 6180
cacccagtat tctactggtc aagtcagcgt ggagatcgag tgggagctgc agaaggaaaa 6240
cagcaagcgc tggaacccgg agatccagta cacttccaac tattacaagt ctaataatgt 6300
tgaatttgct gttaatactg aaggtgtata tagtgaaccc cgccccattg gcaccagata 6360
cctgactcgt aatctgtaag tcgacttgct tgttaatcaa taaaccgttt aattcgtttc 6420
agttgaactt tggtctctgc gaagggcaat tcgtttaaac ctgcaggact agaggtcctg 6480
tattagaggt cacgtgagtg ttttgcgaca ttttgcgaca ccatgtggtc acgctgggta 6540
tttaagcccg agtgagcacg cagggtctcc attttgaagc gggaggtttg aacgcgcagc 6600
cgccaagccg aattctgcag atatcacatg tcctaggaac tatcgatcca tcacactggc 6660
ggccgctcga ctagagcggc cgccaccgcg gtggagctcc agcttttgcg gaccgaatcg 6720
gaaagaacat gtgagcaaaa ggccagcaaa aggccaggaa ccgtaaaaag gccgcgttgc 6780
tggcgttttt ccataggctc cgcccccctg acgagcatca caaaaatcga cgctcaagtc 6840
agaggtggcg aaacccgaca ggactataaa gataccaggc gtttccccct ggaagctccc 6900
tcgtgcgctc tcctgttccg accctgccgc ttaccggata cctgtccgcc tttctccctt 6960
cgggaagcgt ggcgctttct catagctcac gctgtaggta tctcagttcg gtgtaggtcg 7020
ttcgctccaa gctgggctgt gtgcacgaac cccccgttca gcccgaccgc tgcgccttat 7080
ccggtaacta tcgtcttgag tccaacccgg taagacacga cttatcgcca ctggcagcag 7140
ccactggtaa caggattagc agagcgaggt atgtaggcgg tgctacagag ttcttgaagt 7200
ggtggcctaa ctacggctac actagaagaa cagtatttgg tatctgcgct ctgctgaagc 7260
cagttacctt cggaaaaaga gttggtagct cttgatccgg caaacaaacc accgctggta 7320
gcggtggttt ttttgtttgc aagcagcaga ttacgcgcag aaaaaaagga tctcaagaag 7380
atcctttgat cttttctacg gggtctgacg ctcagtggaa cgaaaactca cgttaaggga 7440
ttttggtcat gagattatca aaaaggatct tcacctagat ccttttaaat taaaaatgaa 7500
gttttaaatc aatctaaagt atatatgagt aaacttggtc tgacagttac caatgcttaa 7560
tcagtgaggc acctatctca gcgatctgtc tatttcgttc atccatagtt gcctgactcc 7620
ccgtcgtgta gataactacg atacgggagg gcttaccatc tggccccagt gctgcaatga 7680
taccgcgaga cccacgctca ccggctccag atttatcagc aataaaccag ccagccggaa 7740
gggccgagcg cagaagtggt cctgcaactt tatccgcctc catccagtct attaattgtt 7800
gccgggaagc tagagtaagt agttcgccag ttaatagttt gcgcaacgtt gttgccattg 7860
ctacaggcat cgtggtgtca cgctcgtcgt ttggtatggc ttcattcagc tccggttccc 7920
aacgatcaag gcgagttaca tgatccccca tgttgtgcaa aaaagcggtt agctccttcg 7980
gtcctccgat cgttgtcaga agtaagttgg ccgcagtgtt atcactcatg gttatggcag 8040
cactgcataa ttctcttact gtcatgccat ccgtaagatg cttttctgtg actggtgagt 8100
actcaaccaa gtcattctga gaatagtgta tgcggcgacc gagttgctct tgcccggcgt 8160
caatacggga taataccgcg ccacatagca gaactttaaa agtgctcatc attggaaaac 8220
gttcttcggg gcgaaaactc tcaaggatct taccgctgtt gagatccagt tcgatgtaac 8280
ccactcgtgc acccaactga tcttcagcat cttttacttt caccagcgtt tctgggtgag 8340
caaaaacagg aaggcaaaat gccgcaaaaa agggaataag ggcgacacgg aaatgttgaa 8400
tactcatact cttccttttt caatattatt gaagcattta tcagggttat tgtctcatga 8460
gcggatacat atttgaatgt atttagaaaa ataaacaaat aggggttccg cgcacatttc 8520
cccgaaaagt gccacctgac gtc 8543
<210> 29
<211> 5262
<212> DNA
<213> Homo sapiens
<400> 29
gtgactctgg cccctactgg gcctcattcc ctggaccctg gtctctcctt cctgaagtca 60
ttgctctcca ctctggacca ggctccccag ggctccctga gccgctcacg gttctttaca 120
ttcctggcca acatttcttc ttcctttgag cctgggagaa tgggggaagg accagtagga 180
gagcccccac ctctccagcc gcctgctctg cggctccatg attttctagt gacactgaga 240
ggtagccccg actgggagcc aatgctaggg ctgctagggg atatgctggc actgctggga 300
caggagcaga ctccccgaga tttcctggtg caccaggcag gggtgctggg tggacttgtg 360
gaggtgctgc tgggagcctt agttcctggg ggccccccta ccccaactcg gcccccatgc 420
acccgtgatg ggccgtctga ctgtgtcctg gctgctgact ggttgccttc tctgctgctg 480
ttgttagagg gcacacgctg gcaagctctg gtgcaggtgc agcccagtgt ggaccccacc 540
aatgccacag gcctcgatgg gagggaggca gctcctcact ttttgcaggg tctgttgggt 600
ttgcttaccc caacagggga gctaggctcc aaggaggctc tttggggcgg tctgctacgc 660
acagtggggg cccccctcta tgctgccttt caggaggggc tgctccgtgt cactcactcc 720
ctgcaggatg aggtcttctc cattttgggg cagccagagc ctgataccaa tgggcagtgc 780
cagggaggta accttcaaca gctgctctta tggggcgtcc ggcacaacct ttcctgggat 840
gtccaggcgc tgggctttct gtctggatca ccacccccac cccctgccct ccttcactgc 900
ctgagcacgg gcgtgcctct gcccagagct tctcagccgt cagcccacat cagcccacgc 960
caacggcgag ccatcactgt ggaggccctc tgtgagaacc acttaggccc agcaccaccc 1020
tacagcattt ccaacttctc catccacttg ctctgccagc acaccaagcc tgccactcca 1080
cagccccatc ccagcaccac tgccatctgc cagacagctg tgtggtatgc agtgtcctgg 1140
gcaccaggtg cccaaggctg gctacaggcc tgccacgacc agtttcctga tgagtttttg 1200
gatgcgatct gcagtaacct ctccttttca gccctgtctg gctccaaccg ccgcctggtg 1260
aagcggctct gtgctggcct gctcccaccc cctaccagct gccctgaagg cctgccccct 1320
gttcccctca ccccagacat cttttggggc tgcttcttgg agaatgagac tctgtgggct 1380
gagcgactgt gtggggaggc aagtctacag gctgtgcccc ccagcaacca ggcttgggtc 1440
cagcatgtgt gccagggccc caccccagat gtcactgcct ccccaccatg ccacattgga 1500
ccctgtgggg aacgctgccc ggatgggggc agcttcctgg tgatggtctg tgccaatgac 1560
accatgtatg aggtcctggt gcccttctgg ccttggctag caggccaatg caggataagt 1620
cgtgggggca atgacacttg cttcctagaa gggctgctgg gcccccttct gccctctctg 1680
ccaccactgg gaccatcccc actctgtctg acccctggcc ccttcctcct tggcatgcta 1740
tcccagttgc cacgctgtca gtcctctgtc ccagctcttg ctcaccccac acgcctacac 1800
tatctcctcc gcctgctgac cttcctcttg ggtccagggg ctgggggcgc tgaggcccag 1860
gggatgctgg gtcgggccct actgctctcc agtctcccag acaactgctc cttctgggat 1920
gcctttcgcc cagagggccg gcgcagtgtg ctacggacga ttggggaata cctggaacaa 1980
gatgaggagc agccaacccc atcaggcttt gaacccactg tcaaccccag ctctggtata 2040
agcaagatgg agctgctggc ctgctttagt cctgtgctgt gggatctgct ccagagggaa 2100
aagagtgttt gggccctgca gattctagtg caggcgtacc tgcatatgcc cccagaaaac 2160
ctccagcagc tggtgctttc agcagagagg gaggctgcac agggcttcct gacactcatg 2220
ctgcagggga agctgcaggg gaagctgcag gtaccaccat ccgaggagca ggccctgggt 2280
cgcctgacag ccctgctgct ccagcggtac ccacgcctca cctcccagct cttcattgac 2340
ctgtcaccac tcatcccttt cttggctgtc tctgacctga tgcgcttccc accatccctg 2400
ttagccaacg acagtgtcct ggctgccatc cgggattaca gcccaggaat gaggcctgaa 2460
cagaaggagg ctctggcaaa gcgactgctg gcccctgaac tgtttgggga agtgcctgcc 2520
tggccccagg agctgctgtg ggcagtgctg cccctgctcc cccacctccc tctggagaac 2580
tttttgcagc tcagccctca ccagatccag gccctggagg atagctggcc agcagcaggt 2640
ctggggccag ggcatgcccg ccatgtgctg cgcagcctgg taaaccagag tgtccaggat 2700
ggtgaggagc aggtacgcag gcttgggccc ctcgcctgtt tcctgagccc tgaggagctg 2760
cagagcctag tgcccctgag tgatccaacg gggccagtag aacgggggct gctggaatgt 2820
gcagccaatg ggaccctcag cccagaagga cgggtggcat atgaacttct gggtgtgttg 2880
cgctcatctg gaggagcggt gctgagcccc cgggagctgc gggtctgggc ccctctcttc 2940
tctcagctgg gcctccgctt ccttcaggag ctgtcagagc cccagcttag agccatgctt 3000
cctgtcctgc agggaactag tgttacacct gctcaggctg tcctgctgct tggacggctc 3060
cttcctaggc acgatctatc cctggaggaa ctctgctcct tgcaccttct gctaccaggc 3120
ctcagccccc agacactcca ggccatccct aggcgagtcc tggtcggggc ttgttcctgc 3180
ctggcccctg aactgtcacg cctctcagcc tgccagaccg cagcactgct gcagaccttt 3240
cgggttaaag atggtgttaa aaatatgggt acaacaggtg ctggtccagc tgtgtgtatc 3300
cctggtcagc ctattcccac cacctggcca gactgcctgc ttcccctgct cccattaaag 3360
ctgctacaac tggattcctt ggctcttctg gcaaatcgaa gacgctactg ggagctgccc 3420
tggtctgagc agcaggcaca gtttctctgg aagaagatgc aagtacccac caaccttacc 3480
ctcaggaatc tgcaggctct gggcaccctg gcaggaggca tgtcctgtga gtttctgcag 3540
cagatcaact ccatggtaga cttccttgaa gtggtgcaca tgatctatca gctgcccact 3600
agagttcgag ggagcctgag ggcctgtatc tgggcagagc tacagcggag gatggcaatg 3660
ccagaaccag aatggacaac tgtagggcca gaactgaacg ggctggatag caagctactc 3720
ctggacttac cgatccagtt gatggacaga ctatccaatg aatccattat gttggtggtg 3780
gagctggtgc aaagagctcc agagcagctg ctggcactga cccccctcca ccaggcagcc 3840
ctggcagaga gggcactaca aaacctggct ccaaaggaga ctccagtctc aggggaagtg 3900
ctggagacct taggcccttt ggttggattc ctggggacag agagcacacg acagatcccc 3960
ctacagatcc tgctgtccca tctcagtcag ctgcaaggct tctgcctagg agagacattt 4020
gccacagagc tgggatggct gctattgcag gagtctgttc ttgggaaacc agagttgtgg 4080
agccaggatg aagtagagca agctggacgc ctagtattca ctctgtctac tgaggcaatt 4140
tccttgatcc ccagggaggc cttgggtcca gagaccctgg agcggcttct agaaaagcag 4200
cagagctggg agcagagcag agttggacag ctgtgtaggg agccacagct tgctgccaag 4260
aaagcagccc tggtagcagg ggtggtgcga ccagctgctg aggatcttcc agaacctgtg 4320
ccaaattgtg cagatgtacg agggacattc ccagcagcct ggtctgcaac ccagattgca 4380
gagatggagc tctcagactt tgaggactgc ctgacattat ttgcaggaga cccaggactt 4440
gggcctgagg aactgcgggc agccatgggc aaagcaaaac agttgtgggg tcccccccgg 4500
ggatttcgtc ctgagcagat cctgcagctt ggtaggctct taataggtct aggagatcgg 4560
gaactacagg agctgatcct agtggactgg ggagtgctga gcaccctggg gcagatagat 4620
ggctggagca ccactcagct ccgcattgtg gtctccagtt tcctacggca gagtggtcgg 4680
catgtgagcc acctggactt cgttcatctg acagcgctgg gttatactct ctgtggactg 4740
cggccagagg agctccagca catcagcagt tgggagttca gccaagcagc tctcttcctc 4800
ggcaccctgc atctccagtg ctctgaggaa caactggagg ttctggccca cctacttgta 4860
ctgcctggtg ggtttggccc aatcagtaac tgggggcctg agatcttcac tgaaattggc 4920
accatagcag ctgggatccc agacctggct ctttcagcac tgctgcgggg acagatccag 4980
ggcgttactc ctcttgccat ttctgtcatc cctcctccta aatttgctgt ggtgtttagt 5040
cccatccaac tatctagtct caccagtgct caggctgtgg ctgtcactcc tgagcaaatg 5100
gcctttctga gtcctgagca gcgacgagca gttgcatggg cccaacatga gggaaaggag 5160
agcccagaac agcaaggtcg aagtacagcc tggggcctcc aggactggtc acgaccttcc 5220
tggtccctgg tattgactat cagcttcctt ggccacctgc ta 5262
<210> 30
<211> 5515
<212> DNA
<213> Homo sapiens
<400> 30
gccctgccct cacctggcta tcccacacag gtgagaataa ccagaactca cctccggtac 60
cagtgttcac ttggaaacat ggctctcagc ctctggcccc tgctgctgct gctgctgctg 120
ctgctgctgc tgtcctttgc agtgactctg gcccctactg ggcctcattc cctggaccct 180
ggtctctcct tcctgaagtc attgctctcc actctggacc aggctcccca gggctccctg 240
agccgctcac ggttctttac attcctggcc aacatttctt cttcctttga gcctgggaga 300
atgggggaag gaccagtagg agagccccca cctctccagc cgcctgctct gcggctccat 360
gattttctag tgacactgag aggtagcccc gactgggagc caatgctagg gctgctaggg 420
gatatgctgg cactgctggg acaggagcag actccccgag atttcctggt gcaccaggca 480
ggggtgctgg gtggacttgt ggaggtgctg ctgggagcct tagttcctgg gggcccccct 540
accccaactc ggcccccatg cacccgtgat gggccgtctg actgtgtcct ggctgctgac 600
tggttgcctt ctctgctgct gttgttagag ggcacacgct ggcaagctct ggtgcaggtg 660
cagcccagtg tggaccccac caatgccaca ggcctcgatg ggagggaggc agctcctcac 720
tttttgcagg gtctgttggg tttgcttacc ccaacagggg agctaggctc caaggaggct 780
ctttggggcg gtctgctacg cacagtgggg gcccccctct atgctgcctt tcaggagggg 840
ctgctccgtg tcactcactc cctgcaggat gaggtcttct ccattttggg gcagccagag 900
cctgatacca atgggcagtg ccagggaggt aaccttcaac agctgctctt atggggcgtc 960
cggcacaacc tttcctggga tgtccaggcg ctgggctttc tgtctggatc accaccccca 1020
ccccctgccc tccttcactg cctgagcacg ggcgtgcctc tgcccagagc ttctcagccg 1080
tcagcccaca tcagcccacg ccaacggcga gccatcactg tggaggccct ctgtgagaac 1140
cacttaggcc cagcaccacc ctacagcatt tccaacttct ccatccactt gctctgccag 1200
cacaccaagc ctgccactcc acagccccat cccagcacca ctgccatctg ccagacagct 1260
gtgtggtatg cagtgtcctg ggcaccaggt gcccaaggct ggctacaggc ctgccacgac 1320
cagtttcctg atgagttttt ggatgcgatc tgcagtaacc tctccttttc agccctgtct 1380
ggctccaacc gccgcctggt gaagcggctc tgtgctggcc tgctcccacc ccctaccagc 1440
tgccctgaag gcctgccccc tgttcccctc accccagaca tcttttgggg ctgcttcttg 1500
gagaatgaga ctctgtgggc tgagcgactg tgtggggagg caagtctaca ggctgtgccc 1560
cccagcaacc aggcttgggt ccagcatgtg tgccagggcc ccaccccaga tgtcactgcc 1620
tccccaccat gccacattgg accctgtggg gaacgctgcc cggatggggg cagcttcctg 1680
gtgatggtct gtgccaatga caccatgtat gaggtcctgg tgcccttctg gccttggcta 1740
gcaggccaat gcaggataag tcgtgggggc aatgacactt gcttcctaga agggctgctg 1800
ggcccccttc tgccctctct gccaccactg ggaccatccc cactctgtct gacccctggc 1860
cccttcctcc ttggcatgct atcccagttg ccacgctgtc agtcctctgt cccagctctt 1920
gctcacccca cacgcctaca ctatctcctc cgcctgctga ccttcctctt gggtccaggg 1980
gctgggggcg ctgaggccca ggggatgctg ggtcgggccc tactgctctc cagtctccca 2040
gacaactgct ccttctggga tgcctttcgc ccagagggcc ggcgcagtgt gctacggacg 2100
attggggaat acctggaaca agatgaggag cagccaaccc catcaggctt tgaacccact 2160
gtcaacccca gctctggtat aagcaagatg gagctgctgg cctgctttag tcctgtgctg 2220
tgggatctgc tccagaggga aaagagtgtt tgggccctgc agattctagt gcaggcgtac 2280
ctgcatatgc ccccagaaaa cctccagcag ctggtgcttt cagcagagag ggaggctgca 2340
cagggcttcc tgacactcat gctgcagggg aagctgcagg ggaagctgca ggtaccacca 2400
tccgaggagc aggccctggg tcgcctgaca gccctgctgc tccagcggta cccacgcctc 2460
acctcccagc tcttcattga cctgtcacca ctcatccctt tcttggctgt ctctgacctg 2520
atgcgcttcc caccatccct gttagccaac gacagtgtcc tggctgccat ccgggattac 2580
agcccaggaa tgaggcctga acagaaggag gctctggcaa agcgactgct ggcccctgaa 2640
ctgtttgggg aagtgcctgc ctggccccag gagctgctgt gggcagtgct gcccctgctc 2700
ccccacctcc ctctggagaa ctttttgcag ctcagccctc accagatcca ggccctggag 2760
gatagctggc cagcagcagg tctggggcca gggcatgccc gccatgtgct gcgcagcctg 2820
gtaaaccaga gtgtccagga tggtgaggag caggtacgca ggcttgggcc cctcgcctgt 2880
ttcctgagcc ctgaggagct gcagagccta gtgcccctga gtgatccaac ggggccagta 2940
gaacgggggc tgctggaatg tgcagccaat gggaccctca gcccagaagg acgggtggca 3000
tatgaacttc tgggtgtgtt gcgctcatct ggaggagcgg tgctgagccc ccgggagctg 3060
cgggtctggg cccctctctt ctctcagctg ggcctccgct tccttcagga gctgtcagag 3120
ccccagctta gagccatgct tcctgtcctg cagggaacta gtgttacacc tgctcaggct 3180
gtcctgctgc ttggacggct ccttcctagg cacgatctat ccctggagga actctgctcc 3240
ttgcaccttc tgctaccagg cctcagcccc cagacactcc aggccatccc taggcgagtc 3300
ctggtcgggg cttgttcctg cctggcccct gaactgtcac gcctctcagc ctgccagacc 3360
gcagcactgc tgcagacctt tcgggttaaa gatggtgtta aaaatatggg tacaacaggt 3420
gctggtccag ctgtgtgtat ccctggtcag cctattccca ccacctggcc agactgcctg 3480
cttcccctgc tcccattaaa gctgctacaa ctggattcct tggctcttct ggcaaatcga 3540
agacgctact gggagctgcc ctggtctgag cagcaggcac agtttctctg gaagaagatg 3600
caagtaccca ccaaccttac cctcaggaat ctgcaggctc tgggcaccct ggcaggaggc 3660
atgtcctgtg agtttctgca gcagatcaac tccatggtag acttccttga agtggtgcac 3720
atgatctatc agctgcccac tagagttcga gggagcctga gggcctgtat ctgggcagag 3780
ctacagcgga ggatggcaat gccagaacca gaatggacaa ctgtagggcc agaactgaac 3840
gggctggata gcaagctact cctggactta ccgatccagt tgatggacag actatccaat 3900
gaatccatta tgttggtggt ggagctggtg caaagagctc cagagcagct gctggcactg 3960
acccccctcc accaggcagc cctggcagag agggcactac aaaacctggc tccaaaggag 4020
actccagtct caggggaagt gctggagacc ttaggccctt tggttggatt cctggggaca 4080
gagagcacac gacagatccc cctacagatc ctgctgtccc atctcagtca gctgcaaggc 4140
ttctgcctag gagagacatt tgccacagag ctgggatggc tgctattgca ggagtctgtt 4200
cttgggaaac cagagttgtg gagccaggat gaagtagagc aagctggacg cctagtattc 4260
actctgtcta ctgaggcaat ttccttgatc cccagggagg ccttgggtcc agagaccctg 4320
gagcggcttc tagaaaagca gcagagctgg gagcagagca gagttggaca gctgtgtagg 4380
gagccacagc ttgctgccaa gaaagcagcc ctggtagcag gggtggtgcg accagctgct 4440
gaggatcttc cagaacctgt gccaaattgt gcagatgtac gagggacatt cccagcagcc 4500
tggtctgcaa cccagattgc agagatggag ctctcagact ttgaggactg cctgacatta 4560
tttgcaggag acccaggact tgggcctgag gaactgcggg cagccatggg caaagcaaaa 4620
cagttgtggg gtcccccccg gggatttcgt cctgagcaga tcctgcagct tggtaggctc 4680
ttaataggtc taggagatcg ggaactacag gagctgatcc tagtggactg gggagtgctg 4740
agcaccctgg ggcagataga tggctggagc accactcagc tccgcattgt ggtctccagt 4800
ttcctacggc agagtggtcg gcatgtgagc cacctggact tcgttcatct gacagcgctg 4860
ggttatactc tctgtggact gcggccagag gagctccagc acatcagcag ttgggagttc 4920
agccaagcag ctctcttcct cggcaccctg catctccagt gctctgagga acaactggag 4980
gttctggccc acctacttgt actgcctggt gggtttggcc caatcagtaa ctgggggcct 5040
gagatcttca ctgaaattgg caccatagca gctgggatcc cagacctggc tctttcagca 5100
ctgctgcggg gacagatcca gggcgttact cctcttgcca tttctgtcat ccctcctcct 5160
aaatttgctg tggtgtttag tcccatccaa ctatctagtc tcaccagtgc tcaggctgtg 5220
gctgtcactc ctgagcaaat ggcctttctg agtcctgagc agcgacgagc agttgcatgg 5280
gcccaacatg agggaaagga gagcccagaa cagcaaggtc gaagtacagc ctggggcctc 5340
caggactggt cacgaccttc ctggtccctg gtattgacta tcagcttcct tggccacctg 5400
ctatgagcct gtctctacag tagaaggaga ttgtggggag agaaatctta agtcataatg 5460
aataaagtgc aaacagaagt gcatcctgat tattttcaga agctgatgag gaata 5515
<210> 31
<211> 5361
<212> DNA
<213> Mus musculus
<400> 31
gcccctactg ggcctcagtc tttggatgct ggtctctccc ttctgaagtc attcgtagcc 60
actctggacc aagctcctca gcgttccctc agccagtcac ggttctctgc gttcctggcc 120
aacatttctt catccttcca gcttgggagg atgggggagg gaccggtggg agagccccca 180
cctctccagc cccctgcact tcgacttcat gatttcctcg tgacactgag aggtagccca 240
gactgggagc caatgctagg gcttctggga gatgtgctgg cactcctggg acaggaacag 300
actccccggg actttttggt gcaccaggca ggtgtactgg gtggacttgt agaggcattg 360
ttgggagcgt tagttcctgg aggcccccct gcccccactc gacccccatg cacccgtgat 420
ggcccttctg actgtgtcct ggctgctgat tggttgcctt ctctgatgtt gttattagag 480
ggtacacgct ggcaggccct ggtgcagttg cagcccagtg tggacccaac caatgccaca 540
ggtcttgatg gtagagagcc agctcctcac tttttacagg gtctgctggg cttgcttacc 600
ccagcaggag agttgggctc tgaggaggct ctttggggtg gtctgctgcg cacagtgggg 660
gcccccctct atgctgcctt ccaggagggg ctactgcgag tcactcattc tctgcaagat 720
gaggtctttt ctattatggg acagccagag cctgatgcca gtgggcagtg ccagggaggc 780
aaccttcaac agctgctttt atggggcatg cggaacaacc tttcttggga cgcccgagca 840
ctgggttttc tatctggatc accacctcca ccccctgctc tcctgcactg cctgagcaga 900
ggtgtgcctc tgcccagggc ttcccagcct gcggctcaca tcagccctcg acagcggcga 960
gccatctctg tggaggccct ctgcgagaac cactcaggcc cagagccacc ctacagcatc 1020
tccaacttct ccatctactt gctctgccag cacatcaagc ctgccacccc gcggccccct 1080
cctaccaccc cacggcctcc tcctaccacc ccacagcccc ctcctaccac tacacagccc 1140
attcctgaca ctacacagcc ccctcctgtc accccaaggc ctcctcctac caccccacaa 1200
ccccctccta gcacagctgt catctgccag acagctgtat ggtacgcagt ctcgtgggca 1260
ccaggtgccc gaggttggct ccaagcctgc catgatcagt ttcctgatca atttctggat 1320
atgatctgcg gcaacctctc attttcagcc ctgtctggcc ccagtcgtcc tttggtaaag 1380
cagctctgtg ctggcttgct cccacccccc actagctgtc caccaggcct gatccctgtg 1440
cccctcaccc cagaaatatt ctggggctgt ttcctggaga atgagacact gtgggctgaa 1500
cggttgtgtg tggaggacag tctgcaggct gtgcccccga ggaaccaggc ttgggttcag 1560
catgtgtgtc ggggccccac cttggacgcc actgattttc caccgtgccg cgttggaccc 1620
tgtggggaac gctgcccaga tgggggcagc ttcctgctca tggtctgtgc caatgacact 1680
ctgtatgaag ccttggttcc cttctgggct tggctagcag gccaatgcag aattagtcgt 1740
ggaggaaatg atacttgctt tctagaaggc atgctgggcc ccttgttgcc ctctctgccc 1800
cctctgggac catccccact ctgtctggct cctggtcctt ttctgcttgg catgttatcc 1860
cagttgccac gctgtcagtc ctccgtgcca gccctcgccc accccacgcg cctacattac 1920
ctcctgcgcc tactgacctt ccttctgggt ccagggactg ggggtgccga gacgcagggg 1980
atgttaggtc aagccctgct gctctctagt ctcccagaca actgttcatt ctgggatgcc 2040
ttccgcccag agggccggag aagtgtactg aggacagtcg gagagtactt gcagcgggaa 2100
gagccaaccc caccaggctt agactcctcc ctcagcctcg gctctggtat gagcaagatg 2160
gagcttctgt cctgcttcag tcctgtactg tgggatctac tccagagaga gaagagcgtt 2220
tgggccctga ggaccctggt gaaggcctac ctgcgcatgc ctccagaaga ccttcagcag 2280
cttgtgcttt cagcagagat ggaggctgca cagggcttcc tgacgctcat gcttcgttcc 2340
tgggctaagc tgaaggttca accatccgag gagcaggcca tgggccgcct gacagccttg 2400
ctgctccagc ggtacccacg cctcacctcc caactcttta tcgacatgtc accgctcatc 2460
cccttcctgg ctgtccctga cctcatgcgc ttcccaccgt cccttttggc caacgacagt 2520
gtcctggctg ccatcaggga tcacagctca ggaatgaagc ctgaacagaa ggaggccctg 2580
gcaaaacgac tgctggcccc tgagctgttt ggagaagtgc ctgattggcc ccaggagctg 2640
ctgtgggcag ccctgcctct gcttccccat ctgcctctgg agagctttct ccagctcagc 2700
cctcaccaga tccaggccct ggaggatagc tggccagtag cagatcttgg gccgggacac 2760
gcccgacatg tgcttcgtag cctagtaaac cagagcatgg aggatgggga ggagcaggtg 2820
ctcaggcttg ggtccctcgc ctgtttcctg agtcctgagg agctacagag tctggtgccc 2880
ttgagtgatc caatggggcc tgtagaacag ggtctgctgg aatgtgcggc caatgggacc 2940
ctcagcccag aaggacgggt ggcatatgaa cttctgggag tgttgcgttc atctggagga 3000
actgtcttaa gcccccgaga gctgagggtc tgggcacctc tctttcccca gctgggcctc 3060
cgcttcctgc aggagctctc agagacccag cttagagcca tgcttcctgc cctacaggga 3120
gccagtgtca cacctgccca ggctgttctg ttgtttggaa ggctccttcc taagcatgat 3180
ctgtccctgg aggaactctg ctccctgcac cctctcctgc caggtctcag cccccagaca 3240
ctccaggcca tccctaagag agttctggtt ggtgcttgtt cctgcctggg ccctgaactg 3300
tcaaggcttt cagcttgcca gattgcagct ctgctgcaga cctttcgggt aaaagatggt 3360
gttaaaaata tgggtgcagc aggtgccggc tcagccgtgt gcattcctgg gcagcccacc 3420
acttggccag actgcctgct tcccctgctc ccattaaagc tgctacagct ggacgctgca 3480
gctcttctgg caaaccgaag actctatcgg cagctgcctt ggtctgagca acaggcacag 3540
tttctctgga agaaaatgca agtgcctacc aacctgagcc tgaggaatct gcaggctctg 3600
ggcaacttgg caggaggcat gacctgcgag tttctgcagc agatcagctc aatggttgac 3660
tttcttgatg tggtacacat gctctaccag ctgcccactg gtgttcgaga gagcctgcgg 3720
gcctgtatct ggacagagct acagcggagg atgacaatgc cagagccaga gctgaccacc 3780
ctagggccag aactgagtga acttgacaca aagctactcc tggacttgcc gatccagctg 3840
atggacagat tgtccaatga ttccattatg ttggtggtgg agatggtcca aggcgctcca 3900
gagcagctgc tggcactgac cccactccac cagacagcct tggcagagcg agcacttaaa 3960
aacctggctc caaaggagac cccaatctcc aaagaagtgc tggagacact gggccccttg 4020
gttggattcc tgggaataga gagcacgcga cggatccctt tacccattct actgtctcat 4080
ctcagtcagc tgcagggctt ctgcctagga gagacatttg ccacagagct gggatggctg 4140
ctgttgcagg agcctgttct tggaaaacca gaattgtgga gccaggatga aatagagcaa 4200
gctggacgcc tagtattcac tctgtctgct gaggctattt cctcgatccc cagggaggct 4260
ttgggcccag agacactgga gaggcttctg ggaaagcatc aaagctggga gcagagcaga 4320
gtgggccatc tgtgtgggga gtcacagctt gcccacaaga aagcagctct ggtagctggg 4380
attgtgcatc cagctgctga gggtctccaa gagcctgtac caaactgtgc agacatacgg 4440
ggaaccttcc cagcggcctg gtctgcgaca caaatctcag agatggaact ctcagacttt 4500
gaagactgcc tgtcactatt tgctggagat ccaggacttg gtcctgagga actacgggca 4560
gccatgggca aggccaagca gttgtggggt ccccctcgag gattccgtcc tgagcagatc 4620
ttgcagctgg gccgtctcct gataggtcta ggagaacggg aactgcagga gcttaccttg 4680
gtggactggg gtgtgctgag cagcctgggg caaatagatg gctggagttc catgcagctc 4740
cgagccgtgg tctccagttt cctaaggcag agtggtcggc atgtgagcca cctggacttc 4800
atttatctga cagcactggg ttacacagtc tgtggattgc gaccagagga gttacagcac 4860
atcagcagtt gggagtttag ccaagcagct ctcttcctgg gtagcttgca tctcccgtgc 4920
tctgaggaac agctggaagt tctggcctat ctccttgtgt tgcctggtgg ctttggccca 4980
gtcagtaact gggggcctga gatcttcact gaaattggca caatagcagc tggcatccca 5040
gacctggctc tttcagcatt actgcgggga cagatccaag gcctgactcc tcttgccatt 5100
tctgtcattc ctgctcccaa gtttgcagtg gtcttcaacc ccatccagtt atctagtctc 5160
accaggggtc aggccgtagc tgttactcct gaacagctgg cctatctgag tcctgagcag 5220
cggcgagcag ttgcatgggc ccaacacgaa gggaaggaga tcccagagca gctgggtcga 5280
aactcagcct ggggtctcta cgactggttc caagcctcct gggccctggc attgcccgtc 5340
agcatttttg gccacctatt a 5361
<210> 32
<211> 5757
<212> DNA
<213> Mus musculus
<400> 32
gccccgtctt cacctggcta tcccttcatg gtgagcatag ccagaactca cctctaggcc 60
cagtgtgcac ctggaaatat ggctctgagc ctccagcccc agctgctcct tctcctgtcg 120
ctcctgccgc aggaagtgac ttcagcccct actgggcctc agtctttgga tgctggtctc 180
tcccttctga agtcattcgt agccactctg gaccaagctc ctcagcgttc cctcagccag 240
tcacggttct ctgcgttcct ggccaacatt tcttcatcct tccagcttgg gaggatgggg 300
gagggaccgg tgggagagcc cccacctctc cagccccctg cacttcgact tcatgatttc 360
ctcgtgacac tgagaggtag cccagactgg gagccaatgc tagggcttct gggagatgtg 420
ctggcactcc tgggacagga acagactccc cgggactttt tggtgcacca ggcaggtgta 480
ctgggtggac ttgtagaggc attgttggga gcgttagttc ctggaggccc ccctgccccc 540
actcgacccc catgcacccg tgatggccct tctgactgtg tcctggctgc tgattggttg 600
ccttctctga tgttgttatt agagggtaca cgctggcagg ccctggtgca gttgcagccc 660
agtgtggacc caaccaatgc cacaggtctt gatggtagag agccagctcc tcacttttta 720
cagggtctgc tgggcttgct taccccagca ggagagttgg gctctgagga ggctctttgg 780
ggtggtctgc tgcgcacagt gggggccccc ctctatgctg ccttccagga ggggctactg 840
cgagtcactc attctctgca agatgaggtc ttttctatta tgggacagcc agagcctgat 900
gccagtgggc agtgccaggg aggcaacctt caacagctgc ttttatgggg catgcggaac 960
aacctttctt gggacgcccg agcactgggt tttctatctg gatcaccacc tccaccccct 1020
gctctcctgc actgcctgag cagaggtgtg cctctgccca gggcttccca gcctgcggct 1080
cacatcagcc ctcgacagcg gcgagccatc tctgtggagg ccctctgcga gaaccactca 1140
ggcccagagc caccctacag catctccaac ttctccatct acttgctctg ccagcacatc 1200
aagcctgcca ccccgcggcc ccctcctacc accccacggc ctcctcctac caccccacag 1260
ccccctccta ccactacaca gcccattcct gacactacac agccccctcc tgtcacccca 1320
aggcctcctc ctaccacccc acaaccccct cctagcacag ctgtcatctg ccagacagct 1380
gtatggtacg cagtctcgtg ggcaccaggt gcccgaggtt ggctccaagc ctgccatgat 1440
cagtttcctg atcaatttct ggatatgatc tgcggcaacc tctcattttc agccctgtct 1500
ggccccagtc gtcctttggt aaagcagctc tgtgctggct tgctcccacc ccccactagc 1560
tgtccaccag gcctgatccc tgtgcccctc accccagaaa tattctgggg ctgtttcctg 1620
gagaatgaga cactgtgggc tgaacggttg tgtgtggagg acagtctgca ggctgtgccc 1680
ccgaggaacc aggcttgggt tcagcatgtg tgtcggggcc ccaccttgga cgccactgat 1740
tttccaccgt gccgcgttgg accctgtggg gaacgctgcc cagatggggg cagcttcctg 1800
ctcatggtct gtgccaatga cactctgtat gaagccttgg ttcccttctg ggcttggcta 1860
gcaggccaat gcagaattag tcgtggagga aatgatactt gctttctaga aggcatgctg 1920
ggccccttgt tgccctctct gccccctctg ggaccatccc cactctgtct ggctcctggt 1980
ccttttctgc ttggcatgtt atcccagttg ccacgctgtc agtcctccgt gccagccctc 2040
gcccacccca cgcgcctaca ttacctcctg cgcctactga ccttccttct gggtccaggg 2100
actgggggtg ccgagacgca ggggatgtta ggtcaagccc tgctgctctc tagtctccca 2160
gacaactgtt cattctggga tgccttccgc ccagagggcc ggagaagtgt actgaggaca 2220
gtcggagagt acttgcagcg ggaagagcca accccaccag gcttagactc ctccctcagc 2280
ctcggctctg gtatgagcaa gatggagctt ctgtcctgct tcagtcctgt actgtgggat 2340
ctactccaga gagagaagag cgtttgggcc ctgaggaccc tggtgaaggc ctacctgcgc 2400
atgcctccag aagaccttca gcagcttgtg ctttcagcag agatggaggc tgcacagggc 2460
ttcctgacgc tcatgcttcg ttcctgggct aagctgaagg ttcaaccatc cgaggagcag 2520
gccatgggcc gcctgacagc cttgctgctc cagcggtacc cacgcctcac ctcccaactc 2580
tttatcgaca tgtcaccgct catccccttc ctggctgtcc ctgacctcat gcgcttccca 2640
ccgtcccttt tggccaacga cagtgtcctg gctgccatca gggatcacag ctcaggaatg 2700
aagcctgaac agaaggaggc cctggcaaaa cgactgctgg cccctgagct gtttggagaa 2760
gtgcctgatt ggccccagga gctgctgtgg gcagccctgc ctctgcttcc ccatctgcct 2820
ctggagagct ttctccagct cagccctcac cagatccagg ccctggagga tagctggcca 2880
gtagcagatc ttgggccggg acacgcccga catgtgcttc gtagcctagt aaaccagagc 2940
atggaggatg gggaggagca ggtgctcagg cttgggtccc tcgcctgttt cctgagtcct 3000
gaggagctac agagtctggt gcccttgagt gatccaatgg ggcctgtaga acagggtctg 3060
ctggaatgtg cggccaatgg gaccctcagc ccagaaggac gggtggcata tgaacttctg 3120
ggagtgttgc gttcatctgg aggaactgtc ttaagccccc gagagctgag ggtctgggca 3180
cctctctttc cccagctggg cctccgcttc ctgcaggagc tctcagagac ccagcttaga 3240
gccatgcttc ctgccctaca gggagccagt gtcacacctg cccaggctgt tctgttgttt 3300
ggaaggctcc ttcctaagca tgatctgtcc ctggaggaac tctgctccct gcaccctctc 3360
ctgccaggtc tcagccccca gacactccag gccatcccta agagagttct ggttggtgct 3420
tgttcctgcc tgggccctga actgtcaagg ctttcagctt gccagattgc agctctgctg 3480
cagacctttc gggtaaaaga tggtgttaaa aatatgggtg cagcaggtgc cggctcagcc 3540
gtgtgcattc ctgggcagcc caccacttgg ccagactgcc tgcttcccct gctcccatta 3600
aagctgctac agctggacgc tgcagctctt ctggcaaacc gaagactcta tcggcagctg 3660
ccttggtctg agcaacaggc acagtttctc tggaagaaaa tgcaagtgcc taccaacctg 3720
agcctgagga atctgcaggc tctgggcaac ttggcaggag gcatgacctg cgagtttctg 3780
cagcagatca gctcaatggt tgactttctt gatgtggtac acatgctcta ccagctgccc 3840
actggtgttc gagagagcct gcgggcctgt atctggacag agctacagcg gaggatgaca 3900
atgccagagc cagagctgac caccctaggg ccagaactga gtgaacttga cacaaagcta 3960
ctcctggact tgccgatcca gctgatggac agattgtcca atgattccat tatgttggtg 4020
gtggagatgg tccaaggcgc tccagagcag ctgctggcac tgaccccact ccaccagaca 4080
gccttggcag agcgagcact taaaaacctg gctccaaagg agaccccaat ctccaaagaa 4140
gtgctggaga cactgggccc cttggttgga ttcctgggaa tagagagcac gcgacggatc 4200
cctttaccca ttctactgtc tcatctcagt cagctgcagg gcttctgcct aggagagaca 4260
tttgccacag agctgggatg gctgctgttg caggagcctg ttcttggaaa accagaattg 4320
tggagccagg atgaaataga gcaagctgga cgcctagtat tcactctgtc tgctgaggct 4380
atttcctcga tccccaggga ggctttgggc ccagagacac tggagaggct tctgggaaag 4440
catcaaagct gggagcagag cagagtgggc catctgtgtg gggagtcaca gcttgcccac 4500
aagaaagcag ctctggtagc tgggattgtg catccagctg ctgagggtct ccaagagcct 4560
gtaccaaact gtgcagacat acggggaacc ttcccagcgg cctggtctgc gacacaaatc 4620
tcagagatgg aactctcaga ctttgaagac tgcctgtcac tatttgctgg agatccagga 4680
cttggtcctg aggaactacg ggcagccatg ggcaaggcca agcagttgtg gggtccccct 4740
cgaggattcc gtcctgagca gatcttgcag ctgggccgtc tcctgatagg tctaggagaa 4800
cgggaactgc aggagcttac cttggtggac tggggtgtgc tgagcagcct ggggcaaata 4860
gatggctgga gttccatgca gctccgagcc gtggtctcca gtttcctaag gcagagtggt 4920
cggcatgtga gccacctgga cttcatttat ctgacagcac tgggttacac agtctgtgga 4980
ttgcgaccag aggagttaca gcacatcagc agttgggagt ttagccaagc agctctcttc 5040
ctgggtagct tgcatctccc gtgctctgag gaacagctgg aagttctggc ctatctcctt 5100
gtgttgcctg gtggctttgg cccagtcagt aactgggggc ctgagatctt cactgaaatt 5160
ggcacaatag cagctggcat cccagacctg gctctttcag cattactgcg gggacagatc 5220
caaggcctga ctcctcttgc catttctgtc attcctgctc ccaagtttgc agtggtcttc 5280
aaccccatcc agttatctag tctcaccagg ggtcaggccg tagctgttac tcctgaacag 5340
ctggcctatc tgagtcctga gcagcggcga gcagttgcat gggcccaaca cgaagggaag 5400
gagatcccag agcagctggg tcgaaactca gcctggggtc tctacgactg gttccaagcc 5460
tcctgggccc tggcattgcc cgtcagcatt tttggccacc tattatgata actgttcctt 5520
cagttgaggg agaaaattta catcatactg aacaacttgt aaatggaagt gcatactaat 5580
tattctcagt aagtggatga ggattgtggg taaaattcca atgcattcca cccacctgag 5640
aactgtgctc ctggcatata cgcctcttgc catcatgaat aacctcactg tttcttttca 5700
tttcctactt cctcctcacc acaccaatag aaataacaca gacagctgca acataat 5757
<210> 33
<211> 5379
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 33
atggctctca gcctctggcc cctgctgctg ctgctgctgc tgctgctgct gctgtccttt 60
gcagtgactc tggcccctac tgggcctcat tccctggacc ctggtctctc cttcctgaag 120
tcattgctct ccactctgga ccaggctccc cagggctccc tgagccgctc acggttcttt 180
acattcctgg ccaacatttc ttcttccttt gagcctggga gaatggggga aggaccagta 240
ggagagcccc cacctctcca gccgcctgct ctgcggctcc atgattttct agtgacactg 300
agaggtagcc ccgactggga gccaatgcta gggctgctag gggatatgct ggcactgctg 360
ggacaggagc agactccccg agatttcctg gtgcaccagg caggggtgct gggtggactt 420
gtggaggtgc tgctgggagc cttagttcct gggggccccc ctaccccaac tcggccccca 480
tgcacccgtg atgggccgtc tgactgtgtc ctggctgctg actggttgcc ttctctgctg 540
ctgttgttag agggcacacg ctggcaagct ctggtgcagg tgcagcccag tgtggacccc 600
accaatgcca caggcctcga tgggagggag gcagctcctc actttttgca gggtctgttg 660
ggtttgctta ccccaacagg ggagctaggc tccaaggagg ctctttgggg cggtctgcta 720
cgcacagtgg gggcccccct ctatgctgcc tttcaggagg ggctgctccg tgtcactcac 780
tccctgcagg atgaggtctt ctccattttg gggcagccag agcctgatac caatgggcag 840
tgccagggag gtaaccttca acagctgctc ttatggggcg tccggcacaa cctttcctgg 900
gatgtccagg cgctgggctt tctgtctgga tcaccacccc caccccctgc cctccttcac 960
tgcctgagca cgggcgtgcc tctgcccaga gcttctcagc cgtcagccca catcagccca 1020
cgccaacggc gagccatcac tgtggaggcc ctctgtgaga accacttagg cccagcacca 1080
ccctacagca tttccaactt ctccatccac ttgctctgcc agcacaccaa gcctgccact 1140
ccacagcccc atcccagcac cactgccatc tgccagacag ctgtgtggta tgcagtgtcc 1200
tgggcaccag gtgcccaagg ctggctacag gcctgccacg accagtttcc tgatgagttt 1260
ttggatgcga tctgcagtaa cctctccttt tcagccctgt ctggctccaa ccgccgcctg 1320
gtgaagcggc tctgtgctgg cctgctccca ccccctacca gctgccctga aggcctgccc 1380
cctgttcccc tcaccccaga catcttttgg ggctgcttct tggagaatga gactctgtgg 1440
gctgagcgac tgtgtgggga ggcaagtcta caggctgtgc cccccagcaa ccaggcttgg 1500
gtccagcatg tgtgccaggg ccccacccca gatgtcactg cctccccacc atgccacatt 1560
ggaccctgtg gggaacgctg cccggatggg ggcagcttcc tggtgatggt ctgtgccaat 1620
gacaccatgt atgaggtcct ggtgcccttc tggccttggc tagcaggcca atgcaggata 1680
agtcgtgggg gcaatgacac ttgcttccta gaagggctgc tgggccccct tctgccctct 1740
ctgccaccac tgggaccatc cccactctgt ctgacccctg gccccttcct ccttggcatg 1800
ctatcccagt tgccacgctg tcagtcctct gtcccagctc ttgctcaccc cacacgccta 1860
cactatctcc tccgcctgct gaccttcctc ttgggtccag gggctggggg cgctgaggcc 1920
caggggatgc tgggtcgggc cctactgctc tccagtctcc cagacaactg ctccttctgg 1980
gatgcctttc gcccagaggg ccggcgcagt gtgctacgga cgattgggga atacctggaa 2040
caagatgagg agcagccaac cccatcaggc tttgaaccca ctgtcaaccc cagctctggt 2100
ataagcaaga tggagctgct ggcctgcttt agtcctgtgc tgtgggatct gctccagagg 2160
gaaaagagtg tttgggccct gcagattcta gtgcaggcgt acctgcatat gcccccagaa 2220
aacctccagc agctggtgct ttcagcagag agggaggctg cacagggctt cctgacactc 2280
atgctgcagg ggaagctgca ggggaagctg caggtaccac catccgagga gcaggccctg 2340
ggtcgcctga cagccctgct gctccagcgg tacccacgcc tcacctccca gctcttcatt 2400
gacctgtcac cactcatccc tttcttggct gtctctgacc tgatgcgctt cccaccatcc 2460
ctgttagcca acgacagtgt cctggctgcc atccgggatt acagcccagg aatgaggcct 2520
gaacagaagg aggctctggc aaagcgactg ctggcccctg aactgtttgg ggaagtgcct 2580
gcctggcccc aggagctgct gtgggcagtg ctgcccctgc tcccccacct ccctctggag 2640
aactttttgc agctcagccc tcaccagatc caggccctgg aggatagctg gccagcagca 2700
ggtctggggc cagggcatgc ccgccatgtg ctgcgcagcc tggtaaacca gagtgtccag 2760
gatggtgagg agcaggtacg caggcttggg cccctcgcct gtttcctgag ccctgaggag 2820
ctgcagagcc tagtgcccct gagtgatcca acggggccag tagaacgggg gctgctggaa 2880
tgtgcagcca atgggaccct cagcccagaa ggacgggtgg catatgaact tctgggtgtg 2940
ttgcgctcat ctggaggagc ggtgctgagc ccccgggagc tgcgggtctg ggcccctctc 3000
ttctctcagc tgggcctccg cttccttcag gagctgtcag agccccagct tagagccatg 3060
cttcctgtcc tgcagggaac tagtgttaca cctgctcagg ctgtcctgct gcttggacgg 3120
ctccttccta ggcacgatct atccctggag gaactctgct ccttgcacct tctgctacca 3180
ggcctcagcc cccagacact ccaggccatc cctaggcgag tcctggtcgg ggcttgttcc 3240
tgcctggccc ctgaactgtc acgcctctca gcctgccaga ccgcagcact gctgcagacc 3300
tttcgggtta aagatggtgt taaaaatatg ggtacaacag gtgctggtcc agctgtgtgt 3360
atccctggtc agcctattcc caccacctgg ccagactgcc tgcttcccct gctcccatta 3420
aagctgctac aactggattc cttggctctt ctggcaaatc gaagacgcta ctgggagctg 3480
ccctggtctg agcagcaggc acagtttctc tggaagaaga tgcaagtacc caccaacctt 3540
accctcagga atctgcaggc tctgggcacc ctggcaggag gcatgtcctg tgagtttctg 3600
cagcagatca actccatggt agacttcctt gaagtggtgc acatgatcta tcagctgccc 3660
actagagttc gagggagcct gagggcctgt atctgggcag agctacagcg gaggatggca 3720
atgccagaac cagaatggac aactgtaggg ccagaactga acgggctgga tagcaagcta 3780
ctcctggact taccgatcca gttgatggac agactatcca atgaatccat tatgttggtg 3840
gtggagctgg tgcaaagagc tccagagcag ctgctggcac tgacccccct ccaccaggca 3900
gccctggcag agagggcact acaaaacctg gctccaaagg agactccagt ctcaggggaa 3960
gtgctggaga ccttaggccc tttggttgga ttcctgggga cagagagcac acgacagatc 4020
cccctacaga tcctgctgtc ccatctcagt cagctgcaag gcttctgcct aggagagaca 4080
tttgccacag agctgggatg gctgctattg caggagtctg ttcttgggaa accagagttg 4140
tggagccagg atgaagtaga gcaagctgga cgcctagtat tcactctgtc tactgaggca 4200
atttccttga tccccaggga ggccttgggt ccagagaccc tggagcggct tctagaaaag 4260
cagcagagct gggagcagag cagagttgga cagctgtgta gggagccaca gcttgctgcc 4320
aagaaagcag ccctggtagc aggggtggtg cgaccagctg ctgaggatct tccagaacct 4380
gtgccaaatt gtgcagatgt acgagggaca ttcccagcag cctggtctgc aacccagatt 4440
gcagagatgg agctctcaga ctttgaggac tgcctgacat tatttgcagg agacccagga 4500
cttgggcctg aggaactgcg ggcagccatg ggcaaagcaa aacagttgtg gggtcccccc 4560
cggggatttc gtcctgagca gatcctgcag cttggtaggc tcttaatagg tctaggagat 4620
cgggaactac aggagctgat cctagtggac tggggagtgc tgagcaccct ggggcagata 4680
gatggctgga gcaccactca gctccgcatt gtggtctcca gtttcctacg gcagagtggt 4740
cggcatgtga gccacctgga cttcgttcat ctgacagcgc tgggttatac tctctgtgga 4800
ctgcggccag aggagctcca gcacatcagc agttgggagt tcagccaagc agctctcttc 4860
ctcggcaccc tgcatctcca gtgctctgag gaacaactgg aggttctggc ccacctactt 4920
gtactgcctg gtgggtttgg cccaatcagt aactgggggc ctgagatctt cactgaaatt 4980
ggcaccatag cagctgggat cccagacctg gctctttcag cactgctgcg gggacagatc 5040
cagggcgtta ctcctcttgc catttctgtc atccctcctc ctaaatttgc tgtggtgttt 5100
agtcccatcc aactatctag tctcaccagt gctcaggctg tggctgtcac tcctgagcaa 5160
atggcctttc tgagtcctga gcagcgacga gcagttgcat gggcccaaca tgagggaaag 5220
gagagcccag aacagcaagg tcgaagtaca gcctggggcc tccaggactg gtcacgacct 5280
tcctggtccc tggtattgac tatcagcttc cttggccacc tgctaacgcg tacgcggccg 5340
ctcgagcaga aactcatctc agaagaggat ctgtaatag 5379
<210> 34
<211> 18
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
oligonucleotide
<400> 34
acgcgtacgc ggccgctc 18
<210> 35
<211> 30
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
oligonucleotide
<400> 35
gagcagaaac tcatctcaga agaggatctg 30
<210> 36
<211> 1791
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 36
Met Ala Leu Ser Leu Trp Pro Leu Leu Leu Leu Leu Leu Leu Leu Leu
1 5 10 15
Leu Leu Ser Phe Ala Val Thr Leu Ala Pro Thr Gly Pro His Ser Leu
20 25 30
Asp Pro Gly Leu Ser Phe Leu Lys Ser Leu Leu Ser Thr Leu Asp Gln
35 40 45
Ala Pro Gln Gly Ser Leu Ser Arg Ser Arg Phe Phe Thr Phe Leu Ala
50 55 60
Asn Ile Ser Ser Ser Phe Glu Pro Gly Arg Met Gly Glu Gly Pro Val
65 70 75 80
Gly Glu Pro Pro Pro Leu Gln Pro Pro Ala Leu Arg Leu His Asp Phe
85 90 95
Leu Val Thr Leu Arg Gly Ser Pro Asp Trp Glu Pro Met Leu Gly Leu
100 105 110
Leu Gly Asp Met Leu Ala Leu Leu Gly Gln Glu Gln Thr Pro Arg Asp
115 120 125
Phe Leu Val His Gln Ala Gly Val Leu Gly Gly Leu Val Glu Val Leu
130 135 140
Leu Gly Ala Leu Val Pro Gly Gly Pro Pro Thr Pro Thr Arg Pro Pro
145 150 155 160
Cys Thr Arg Asp Gly Pro Ser Asp Cys Val Leu Ala Ala Asp Trp Leu
165 170 175
Pro Ser Leu Leu Leu Leu Leu Glu Gly Thr Arg Trp Gln Ala Leu Val
180 185 190
Gln Val Gln Pro Ser Val Asp Pro Thr Asn Ala Thr Gly Leu Asp Gly
195 200 205
Arg Glu Ala Ala Pro His Phe Leu Gln Gly Leu Leu Gly Leu Leu Thr
210 215 220
Pro Thr Gly Glu Leu Gly Ser Lys Glu Ala Leu Trp Gly Gly Leu Leu
225 230 235 240
Arg Thr Val Gly Ala Pro Leu Tyr Ala Ala Phe Gln Glu Gly Leu Leu
245 250 255
Arg Val Thr His Ser Leu Gln Asp Glu Val Phe Ser Ile Leu Gly Gln
260 265 270
Pro Glu Pro Asp Thr Asn Gly Gln Cys Gln Gly Gly Asn Leu Gln Gln
275 280 285
Leu Leu Leu Trp Gly Val Arg His Asn Leu Ser Trp Asp Val Gln Ala
290 295 300
Leu Gly Phe Leu Ser Gly Ser Pro Pro Pro Pro Pro Ala Leu Leu His
305 310 315 320
Cys Leu Ser Thr Gly Val Pro Leu Pro Arg Ala Ser Gln Pro Ser Ala
325 330 335
His Ile Ser Pro Arg Gln Arg Arg Ala Ile Thr Val Glu Ala Leu Cys
340 345 350
Glu Asn His Leu Gly Pro Ala Pro Pro Tyr Ser Ile Ser Asn Phe Ser
355 360 365
Ile His Leu Leu Cys Gln His Thr Lys Pro Ala Thr Pro Gln Pro His
370 375 380
Pro Ser Thr Thr Ala Ile Cys Gln Thr Ala Val Trp Tyr Ala Val Ser
385 390 395 400
Trp Ala Pro Gly Ala Gln Gly Trp Leu Gln Ala Cys His Asp Gln Phe
405 410 415
Pro Asp Glu Phe Leu Asp Ala Ile Cys Ser Asn Leu Ser Phe Ser Ala
420 425 430
Leu Ser Gly Ser Asn Arg Arg Leu Val Lys Arg Leu Cys Ala Gly Leu
435 440 445
Leu Pro Pro Pro Thr Ser Cys Pro Glu Gly Leu Pro Pro Val Pro Leu
450 455 460
Thr Pro Asp Ile Phe Trp Gly Cys Phe Leu Glu Asn Glu Thr Leu Trp
465 470 475 480
Ala Glu Arg Leu Cys Gly Glu Ala Ser Leu Gln Ala Val Pro Pro Ser
485 490 495
Asn Gln Ala Trp Val Gln His Val Cys Gln Gly Pro Thr Pro Asp Val
500 505 510
Thr Ala Ser Pro Pro Cys His Ile Gly Pro Cys Gly Glu Arg Cys Pro
515 520 525
Asp Gly Gly Ser Phe Leu Val Met Val Cys Ala Asn Asp Thr Met Tyr
530 535 540
Glu Val Leu Val Pro Phe Trp Pro Trp Leu Ala Gly Gln Cys Arg Ile
545 550 555 560
Ser Arg Gly Gly Asn Asp Thr Cys Phe Leu Glu Gly Leu Leu Gly Pro
565 570 575
Leu Leu Pro Ser Leu Pro Pro Leu Gly Pro Ser Pro Leu Cys Leu Thr
580 585 590
Pro Gly Pro Phe Leu Leu Gly Met Leu Ser Gln Leu Pro Arg Cys Gln
595 600 605
Ser Ser Val Pro Ala Leu Ala His Pro Thr Arg Leu His Tyr Leu Leu
610 615 620
Arg Leu Leu Thr Phe Leu Leu Gly Pro Gly Ala Gly Gly Ala Glu Ala
625 630 635 640
Gln Gly Met Leu Gly Arg Ala Leu Leu Leu Ser Ser Leu Pro Asp Asn
645 650 655
Cys Ser Phe Trp Asp Ala Phe Arg Pro Glu Gly Arg Arg Ser Val Leu
660 665 670
Arg Thr Ile Gly Glu Tyr Leu Glu Gln Asp Glu Glu Gln Pro Thr Pro
675 680 685
Ser Gly Phe Glu Pro Thr Val Asn Pro Ser Ser Gly Ile Ser Lys Met
690 695 700
Glu Leu Leu Ala Cys Phe Ser Pro Val Leu Trp Asp Leu Leu Gln Arg
705 710 715 720
Glu Lys Ser Val Trp Ala Leu Gln Ile Leu Val Gln Ala Tyr Leu His
725 730 735
Met Pro Pro Glu Asn Leu Gln Gln Leu Val Leu Ser Ala Glu Arg Glu
740 745 750
Ala Ala Gln Gly Phe Leu Thr Leu Met Leu Gln Gly Lys Leu Gln Gly
755 760 765
Lys Leu Gln Val Pro Pro Ser Glu Glu Gln Ala Leu Gly Arg Leu Thr
770 775 780
Ala Leu Leu Leu Gln Arg Tyr Pro Arg Leu Thr Ser Gln Leu Phe Ile
785 790 795 800
Asp Leu Ser Pro Leu Ile Pro Phe Leu Ala Val Ser Asp Leu Met Arg
805 810 815
Phe Pro Pro Ser Leu Leu Ala Asn Asp Ser Val Leu Ala Ala Ile Arg
820 825 830
Asp Tyr Ser Pro Gly Met Arg Pro Glu Gln Lys Glu Ala Leu Ala Lys
835 840 845
Arg Leu Leu Ala Pro Glu Leu Phe Gly Glu Val Pro Ala Trp Pro Gln
850 855 860
Glu Leu Leu Trp Ala Val Leu Pro Leu Leu Pro His Leu Pro Leu Glu
865 870 875 880
Asn Phe Leu Gln Leu Ser Pro His Gln Ile Gln Ala Leu Glu Asp Ser
885 890 895
Trp Pro Ala Ala Gly Leu Gly Pro Gly His Ala Arg His Val Leu Arg
900 905 910
Ser Leu Val Asn Gln Ser Val Gln Asp Gly Glu Glu Gln Val Arg Arg
915 920 925
Leu Gly Pro Leu Ala Cys Phe Leu Ser Pro Glu Glu Leu Gln Ser Leu
930 935 940
Val Pro Leu Ser Asp Pro Thr Gly Pro Val Glu Arg Gly Leu Leu Glu
945 950 955 960
Cys Ala Ala Asn Gly Thr Leu Ser Pro Glu Gly Arg Val Ala Tyr Glu
965 970 975
Leu Leu Gly Val Leu Arg Ser Ser Gly Gly Ala Val Leu Ser Pro Arg
980 985 990
Glu Leu Arg Val Trp Ala Pro Leu Phe Ser Gln Leu Gly Leu Arg Phe
995 1000 1005
Leu Gln Glu Leu Ser Glu Pro Gln Leu Arg Ala Met Leu Pro Val
1010 1015 1020
Leu Gln Gly Thr Ser Val Thr Pro Ala Gln Ala Val Leu Leu Leu
1025 1030 1035
Gly Arg Leu Leu Pro Arg His Asp Leu Ser Leu Glu Glu Leu Cys
1040 1045 1050
Ser Leu His Leu Leu Leu Pro Gly Leu Ser Pro Gln Thr Leu Gln
1055 1060 1065
Ala Ile Pro Arg Arg Val Leu Val Gly Ala Cys Ser Cys Leu Ala
1070 1075 1080
Pro Glu Leu Ser Arg Leu Ser Ala Cys Gln Thr Ala Ala Leu Leu
1085 1090 1095
Gln Thr Phe Arg Val Lys Asp Gly Val Lys Asn Met Gly Thr Thr
1100 1105 1110
Gly Ala Gly Pro Ala Val Cys Ile Pro Gly Gln Pro Ile Pro Thr
1115 1120 1125
Thr Trp Pro Asp Cys Leu Leu Pro Leu Leu Pro Leu Lys Leu Leu
1130 1135 1140
Gln Leu Asp Ser Leu Ala Leu Leu Ala Asn Arg Arg Arg Tyr Trp
1145 1150 1155
Glu Leu Pro Trp Ser Glu Gln Gln Ala Gln Phe Leu Trp Lys Lys
1160 1165 1170
Met Gln Val Pro Thr Asn Leu Thr Leu Arg Asn Leu Gln Ala Leu
1175 1180 1185
Gly Thr Leu Ala Gly Gly Met Ser Cys Glu Phe Leu Gln Gln Ile
1190 1195 1200
Asn Ser Met Val Asp Phe Leu Glu Val Val His Met Ile Tyr Gln
1205 1210 1215
Leu Pro Thr Arg Val Arg Gly Ser Leu Arg Ala Cys Ile Trp Ala
1220 1225 1230
Glu Leu Gln Arg Arg Met Ala Met Pro Glu Pro Glu Trp Thr Thr
1235 1240 1245
Val Gly Pro Glu Leu Asn Gly Leu Asp Ser Lys Leu Leu Leu Asp
1250 1255 1260
Leu Pro Ile Gln Leu Met Asp Arg Leu Ser Asn Glu Ser Ile Met
1265 1270 1275
Leu Val Val Glu Leu Val Gln Arg Ala Pro Glu Gln Leu Leu Ala
1280 1285 1290
Leu Thr Pro Leu His Gln Ala Ala Leu Ala Glu Arg Ala Leu Gln
1295 1300 1305
Asn Leu Ala Pro Lys Glu Thr Pro Val Ser Gly Glu Val Leu Glu
1310 1315 1320
Thr Leu Gly Pro Leu Val Gly Phe Leu Gly Thr Glu Ser Thr Arg
1325 1330 1335
Gln Ile Pro Leu Gln Ile Leu Leu Ser His Leu Ser Gln Leu Gln
1340 1345 1350
Gly Phe Cys Leu Gly Glu Thr Phe Ala Thr Glu Leu Gly Trp Leu
1355 1360 1365
Leu Leu Gln Glu Ser Val Leu Gly Lys Pro Glu Leu Trp Ser Gln
1370 1375 1380
Asp Glu Val Glu Gln Ala Gly Arg Leu Val Phe Thr Leu Ser Thr
1385 1390 1395
Glu Ala Ile Ser Leu Ile Pro Arg Glu Ala Leu Gly Pro Glu Thr
1400 1405 1410
Leu Glu Arg Leu Leu Glu Lys Gln Gln Ser Trp Glu Gln Ser Arg
1415 1420 1425
Val Gly Gln Leu Cys Arg Glu Pro Gln Leu Ala Ala Lys Lys Ala
1430 1435 1440
Ala Leu Val Ala Gly Val Val Arg Pro Ala Ala Glu Asp Leu Pro
1445 1450 1455
Glu Pro Val Pro Asn Cys Ala Asp Val Arg Gly Thr Phe Pro Ala
1460 1465 1470
Ala Trp Ser Ala Thr Gln Ile Ala Glu Met Glu Leu Ser Asp Phe
1475 1480 1485
Glu Asp Cys Leu Thr Leu Phe Ala Gly Asp Pro Gly Leu Gly Pro
1490 1495 1500
Glu Glu Leu Arg Ala Ala Met Gly Lys Ala Lys Gln Leu Trp Gly
1505 1510 1515
Pro Pro Arg Gly Phe Arg Pro Glu Gln Ile Leu Gln Leu Gly Arg
1520 1525 1530
Leu Leu Ile Gly Leu Gly Asp Arg Glu Leu Gln Glu Leu Ile Leu
1535 1540 1545
Val Asp Trp Gly Val Leu Ser Thr Leu Gly Gln Ile Asp Gly Trp
1550 1555 1560
Ser Thr Thr Gln Leu Arg Ile Val Val Ser Ser Phe Leu Arg Gln
1565 1570 1575
Ser Gly Arg His Val Ser His Leu Asp Phe Val His Leu Thr Ala
1580 1585 1590
Leu Gly Tyr Thr Leu Cys Gly Leu Arg Pro Glu Glu Leu Gln His
1595 1600 1605
Ile Ser Ser Trp Glu Phe Ser Gln Ala Ala Leu Phe Leu Gly Thr
1610 1615 1620
Leu His Leu Gln Cys Ser Glu Glu Gln Leu Glu Val Leu Ala His
1625 1630 1635
Leu Leu Val Leu Pro Gly Gly Phe Gly Pro Ile Ser Asn Trp Gly
1640 1645 1650
Pro Glu Ile Phe Thr Glu Ile Gly Thr Ile Ala Ala Gly Ile Pro
1655 1660 1665
Asp Leu Ala Leu Ser Ala Leu Leu Arg Gly Gln Ile Gln Gly Val
1670 1675 1680
Thr Pro Leu Ala Ile Ser Val Ile Pro Pro Pro Lys Phe Ala Val
1685 1690 1695
Val Phe Ser Pro Ile Gln Leu Ser Ser Leu Thr Ser Ala Gln Ala
1700 1705 1710
Val Ala Val Thr Pro Glu Gln Met Ala Phe Leu Ser Pro Glu Gln
1715 1720 1725
Arg Arg Ala Val Ala Trp Ala Gln His Glu Gly Lys Glu Ser Pro
1730 1735 1740
Glu Gln Gln Gly Arg Ser Thr Ala Trp Gly Leu Gln Asp Trp Ser
1745 1750 1755
Arg Pro Ser Trp Ser Leu Val Leu Thr Ile Ser Phe Leu Gly His
1760 1765 1770
Leu Leu Thr Arg Thr Arg Pro Leu Glu Gln Lys Leu Ile Ser Glu
1775 1780 1785
Glu Asp Leu
1790
<210> 37
<211> 6
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 37
Thr Arg Thr Arg Pro Leu
1 5
<210> 38
<211> 5481
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 38
atggctctga gcctccagcc ccagctgctc cttctcctgt cgctcctgcc gcaggaagtg 60
acttcagccc ctactgggcc tcagtctttg gatgctggtc tctcccttct gaagtcattc 120
gtagccactc tggaccaagc tcctcagcgt tccctcagcc agtcacggtt ctctgcgttc 180
ctggccaaca tttcttcatc cttccagctt gggaggatgg gggagggacc ggtgggagag 240
cccccacctc tccagccccc tgcacttcga cttcatgatt tcctcgtgac actgagaggt 300
agcccagact gggagccaat gctagggctt ctgggagatg tgctggcact cctgggacag 360
gaacagactc cccgggactt tttggtgcac caggcaggtg tactgggtgg acttgtagag 420
gcattgttgg gagcgttagt tcctggaggc ccccctgccc ccactcgacc cccatgcacc 480
cgtgatggcc cttctgactg tgtcctggct gctgattggt tgccttctct gatgttgtta 540
ttagagggta cacgctggca ggccctggtg cagttgcagc ccagtgtgga cccaaccaat 600
gccacaggtc ttgatggtag agagccagct cctcactttt tacagggtct gctgggcttg 660
cttaccccag caggagagtt gggctctgag gaggctcttt ggggtggtct gctgcgcaca 720
gtgggggccc ccctctatgc tgccttccag gaggggctac tgcgagtcac tcattctctg 780
caagatgagg tcttttctat tatgggacag ccagagcctg atgccagtgg gcagtgccag 840
ggaggcaacc ttcaacagct gcttttatgg ggcatgcgga acaacctttc ttgggacgcc 900
cgagcactgg gttttctatc tggatcacca cctccacccc ctgctctcct gcactgcctg 960
agcagaggtg tgcctctgcc cagggcttcc cagcctgcgg ctcacatcag ccctcgacag 1020
cggcgagcca tctctgtgga ggccctctgc gagaaccact caggcccaga gccaccctac 1080
agcatctcca acttctccat ctacttgctc tgccagcaca tcaagcctgc caccccgcgg 1140
ccccctccta ccaccccacg gcctcctcct accaccccac agccccctcc taccactaca 1200
cagcccattc ctgacactac acagccccct cctgtcaccc caaggcctcc tcctaccacc 1260
ccacaacccc ctcctagcac agctgtcatc tgccagacag ctgtatggta cgcagtctcg 1320
tgggcaccag gtgcccgagg ttggctccaa gcctgccatg atcagtttcc tgatcaattt 1380
ctggatatga tctgcggcaa cctctcattt tcagccctgt ctggccccag tcgtcctttg 1440
gtaaagcagc tctgtgctgg cttgctccca ccccccacta gctgtccacc aggcctgatc 1500
cctgtgcccc tcaccccaga aatattctgg ggctgtttcc tggagaatga gacactgtgg 1560
gctgaacggt tgtgtgtgga ggacagtctg caggctgtgc ccccgaggaa ccaggcttgg 1620
gttcagcatg tgtgtcgggg ccccaccttg gacgccactg attttccacc gtgccgcgtt 1680
ggaccctgtg gggaacgctg cccagatggg ggcagcttcc tgctcatggt ctgtgccaat 1740
gacactctgt atgaagcctt ggttcccttc tgggcttggc tagcaggcca atgcagaatt 1800
agtcgtggag gaaatgatac ttgctttcta gaaggcatgc tgggcccctt gttgccctct 1860
ctgccccctc tgggaccatc cccactctgt ctggctcctg gtccttttct gcttggcatg 1920
ttatcccagt tgccacgctg tcagtcctcc gtgccagccc tcgcccaccc cacgcgccta 1980
cattacctcc tgcgcctact gaccttcctt ctgggtccag ggactggggg tgccgagacg 2040
caggggatgt taggtcaagc cctgctgctc tctagtctcc cagacaactg ttcattctgg 2100
gatgccttcc gcccagaggg ccggagaagt gtactgagga cagtcggaga gtacttgcag 2160
cgggaagagc caaccccacc aggcttagac tcctccctca gcctcggctc tggtatgagc 2220
aagatggagc ttctgtcctg cttcagtcct gtactgtggg atctactcca gagagagaag 2280
agcgtttggg ccctgaggac cctggtgaag gcctacctgc gcatgcctcc agaagacctt 2340
cagcagcttg tgctttcagc agagatggag gctgcacagg gcttcctgac gctcatgctt 2400
cgttcctggg ctaagctgaa ggttcaacca tccgaggagc aggccatggg ccgcctgaca 2460
gccttgctgc tccagcggta cccacgcctc acctcccaac tctttatcga catgtcaccg 2520
ctcatcccct tcctggctgt ccctgacctc atgcgcttcc caccgtccct tttggccaac 2580
gacagtgtcc tggctgccat cagggatcac agctcaggaa tgaagcctga acagaaggag 2640
gccctggcaa aacgactgct ggcccctgag ctgtttggag aagtgcctga ttggccccag 2700
gagctgctgt gggcagccct gcctctgctt ccccatctgc ctctggagag ctttctccag 2760
ctcagccctc accagatcca ggccctggag gatagctggc cagtagcaga tcttgggccg 2820
ggacacgccc gacatgtgct tcgtagccta gtaaaccaga gcatggagga tggggaggag 2880
caggtgctca ggcttgggtc cctcgcctgt ttcctgagtc ctgaggagct acagagtctg 2940
gtgcccttga gtgatccaat ggggcctgta gaacagggtc tgctggaatg tgcggccaat 3000
gggaccctca gcccagaagg acgggtggca tatgaacttc tgggagtgtt gcgttcatct 3060
ggaggaactg tcttaagccc ccgagagctg agggtctggg cacctctctt tccccagctg 3120
ggcctccgct tcctgcagga gctctcagag acccagctta gagccatgct tcctgcccta 3180
cagggagcca gtgtcacacc tgcccaggct gttctgttgt ttggaaggct ccttcctaag 3240
catgatctgt ccctggagga actctgctcc ctgcaccctc tcctgccagg tctcagcccc 3300
cagacactcc aggccatccc taagagagtt ctggttggtg cttgttcctg cctgggccct 3360
gaactgtcaa ggctttcagc ttgccagatt gcagctctgc tgcagacctt tcgggtaaaa 3420
gatggtgtta aaaatatggg tgcagcaggt gccggctcag ccgtgtgcat tcctgggcag 3480
cccaccactt ggccagactg cctgcttccc ctgctcccat taaagctgct acagctggac 3540
gctgcagctc ttctggcaaa ccgaagactc tatcggcagc tgccttggtc tgagcaacag 3600
gcacagtttc tctggaagaa aatgcaagtg cctaccaacc tgagcctgag gaatctgcag 3660
gctctgggca acttggcagg aggcatgacc tgcgagtttc tgcagcagat cagctcaatg 3720
gttgactttc ttgatgtggt acacatgctc taccagctgc ccactggtgt tcgagagagc 3780
ctgcgggcct gtatctggac agagctacag cggaggatga caatgccaga gccagagctg 3840
accaccctag ggccagaact gagtgaactt gacacaaagc tactcctgga cttgccgatc 3900
cagctgatgg acagattgtc caatgattcc attatgttgg tggtggagat ggtccaaggc 3960
gctccagagc agctgctggc actgacccca ctccaccaga cagccttggc agagcgagca 4020
cttaaaaacc tggctccaaa ggagacccca atctccaaag aagtgctgga gacactgggc 4080
cccttggttg gattcctggg aatagagagc acgcgacgga tccctttacc cattctactg 4140
tctcatctca gtcagctgca gggcttctgc ctaggagaga catttgccac agagctggga 4200
tggctgctgt tgcaggagcc tgttcttgga aaaccagaat tgtggagcca ggatgaaata 4260
gagcaagctg gacgcctagt attcactctg tctgctgagg ctatttcctc gatccccagg 4320
gaggctttgg gcccagagac actggagagg cttctgggaa agcatcaaag ctgggagcag 4380
agcagagtgg gccatctgtg tggggagtca cagcttgccc acaagaaagc agctctggta 4440
gctgggattg tgcatccagc tgctgagggt ctccaagagc ctgtaccaaa ctgtgcagac 4500
atacggggaa ccttcccagc ggcctggtct gcgacacaaa tctcagagat ggaactctca 4560
gactttgaag actgcctgtc actatttgct ggagatccag gacttggtcc tgaggaacta 4620
cgggcagcca tgggcaaggc caagcagttg tggggtcccc ctcgaggatt ccgtcctgag 4680
cagatcttgc agctgggccg tctcctgata ggtctaggag aacgggaact gcaggagctt 4740
accttggtgg actggggtgt gctgagcagc ctggggcaaa tagatggctg gagttccatg 4800
cagctccgag ccgtggtctc cagtttccta aggcagagtg gtcggcatgt gagccacctg 4860
gacttcattt atctgacagc actgggttac acagtctgtg gattgcgacc agaggagtta 4920
cagcacatca gcagttggga gtttagccaa gcagctctct tcctgggtag cttgcatctc 4980
ccgtgctctg aggaacagct ggaagttctg gcctatctcc ttgtgttgcc tggtggcttt 5040
ggcccagtca gtaactgggg gcctgagatc ttcactgaaa ttggcacaat agcagctggc 5100
atcccagacc tggctctttc agcattactg cggggacaga tccaaggcct gactcctctt 5160
gccatttctg tcattcctgc tcccaagttt gcagtggtct tcaaccccat ccagttatct 5220
agtctcacca ggggtcaggc cgtagctgtt actcctgaac agctggccta tctgagtcct 5280
gagcagcggc gagcagttgc atgggcccaa cacgaaggga aggagatccc agagcagctg 5340
ggtcgaaact cagcctgggg tctctacgac tggttccaag cctcctgggc cctggcattg 5400
cccgtcagca tttttggcca cctattaacg cgtacgcggc cgctcgagca gaaactcatc 5460
tcagaagagg atctgtaata g 5481
<210> 39
<211> 1825
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 39
Met Ala Leu Ser Leu Gln Pro Gln Leu Leu Leu Leu Leu Ser Leu Leu
1 5 10 15
Pro Gln Glu Val Thr Ser Ala Pro Thr Gly Pro Gln Ser Leu Asp Ala
20 25 30
Gly Leu Ser Leu Leu Lys Ser Phe Val Ala Thr Leu Asp Gln Ala Pro
35 40 45
Gln Arg Ser Leu Ser Gln Ser Arg Phe Ser Ala Phe Leu Ala Asn Ile
50 55 60
Ser Ser Ser Phe Gln Leu Gly Arg Met Gly Glu Gly Pro Val Gly Glu
65 70 75 80
Pro Pro Pro Leu Gln Pro Pro Ala Leu Arg Leu His Asp Phe Leu Val
85 90 95
Thr Leu Arg Gly Ser Pro Asp Trp Glu Pro Met Leu Gly Leu Leu Gly
100 105 110
Asp Val Leu Ala Leu Leu Gly Gln Glu Gln Thr Pro Arg Asp Phe Leu
115 120 125
Val His Gln Ala Gly Val Leu Gly Gly Leu Val Glu Ala Leu Leu Gly
130 135 140
Ala Leu Val Pro Gly Gly Pro Pro Ala Pro Thr Arg Pro Pro Cys Thr
145 150 155 160
Arg Asp Gly Pro Ser Asp Cys Val Leu Ala Ala Asp Trp Leu Pro Ser
165 170 175
Leu Met Leu Leu Leu Glu Gly Thr Arg Trp Gln Ala Leu Val Gln Leu
180 185 190
Gln Pro Ser Val Asp Pro Thr Asn Ala Thr Gly Leu Asp Gly Arg Glu
195 200 205
Pro Ala Pro His Phe Leu Gln Gly Leu Leu Gly Leu Leu Thr Pro Ala
210 215 220
Gly Glu Leu Gly Ser Glu Glu Ala Leu Trp Gly Gly Leu Leu Arg Thr
225 230 235 240
Val Gly Ala Pro Leu Tyr Ala Ala Phe Gln Glu Gly Leu Leu Arg Val
245 250 255
Thr His Ser Leu Gln Asp Glu Val Phe Ser Ile Met Gly Gln Pro Glu
260 265 270
Pro Asp Ala Ser Gly Gln Cys Gln Gly Gly Asn Leu Gln Gln Leu Leu
275 280 285
Leu Trp Gly Met Arg Asn Asn Leu Ser Trp Asp Ala Arg Ala Leu Gly
290 295 300
Phe Leu Ser Gly Ser Pro Pro Pro Pro Pro Ala Leu Leu His Cys Leu
305 310 315 320
Ser Arg Gly Val Pro Leu Pro Arg Ala Ser Gln Pro Ala Ala His Ile
325 330 335
Ser Pro Arg Gln Arg Arg Ala Ile Ser Val Glu Ala Leu Cys Glu Asn
340 345 350
His Ser Gly Pro Glu Pro Pro Tyr Ser Ile Ser Asn Phe Ser Ile Tyr
355 360 365
Leu Leu Cys Gln His Ile Lys Pro Ala Thr Pro Arg Pro Pro Pro Thr
370 375 380
Thr Pro Arg Pro Pro Pro Thr Thr Pro Gln Pro Pro Pro Thr Thr Thr
385 390 395 400
Gln Pro Ile Pro Asp Thr Thr Gln Pro Pro Pro Val Thr Pro Arg Pro
405 410 415
Pro Pro Thr Thr Pro Gln Pro Pro Pro Ser Thr Ala Val Ile Cys Gln
420 425 430
Thr Ala Val Trp Tyr Ala Val Ser Trp Ala Pro Gly Ala Arg Gly Trp
435 440 445
Leu Gln Ala Cys His Asp Gln Phe Pro Asp Gln Phe Leu Asp Met Ile
450 455 460
Cys Gly Asn Leu Ser Phe Ser Ala Leu Ser Gly Pro Ser Arg Pro Leu
465 470 475 480
Val Lys Gln Leu Cys Ala Gly Leu Leu Pro Pro Pro Thr Ser Cys Pro
485 490 495
Pro Gly Leu Ile Pro Val Pro Leu Thr Pro Glu Ile Phe Trp Gly Cys
500 505 510
Phe Leu Glu Asn Glu Thr Leu Trp Ala Glu Arg Leu Cys Val Glu Asp
515 520 525
Ser Leu Gln Ala Val Pro Pro Arg Asn Gln Ala Trp Val Gln His Val
530 535 540
Cys Arg Gly Pro Thr Leu Asp Ala Thr Asp Phe Pro Pro Cys Arg Val
545 550 555 560
Gly Pro Cys Gly Glu Arg Cys Pro Asp Gly Gly Ser Phe Leu Leu Met
565 570 575
Val Cys Ala Asn Asp Thr Leu Tyr Glu Ala Leu Val Pro Phe Trp Ala
580 585 590
Trp Leu Ala Gly Gln Cys Arg Ile Ser Arg Gly Gly Asn Asp Thr Cys
595 600 605
Phe Leu Glu Gly Met Leu Gly Pro Leu Leu Pro Ser Leu Pro Pro Leu
610 615 620
Gly Pro Ser Pro Leu Cys Leu Ala Pro Gly Pro Phe Leu Leu Gly Met
625 630 635 640
Leu Ser Gln Leu Pro Arg Cys Gln Ser Ser Val Pro Ala Leu Ala His
645 650 655
Pro Thr Arg Leu His Tyr Leu Leu Arg Leu Leu Thr Phe Leu Leu Gly
660 665 670
Pro Gly Thr Gly Gly Ala Glu Thr Gln Gly Met Leu Gly Gln Ala Leu
675 680 685
Leu Leu Ser Ser Leu Pro Asp Asn Cys Ser Phe Trp Asp Ala Phe Arg
690 695 700
Pro Glu Gly Arg Arg Ser Val Leu Arg Thr Val Gly Glu Tyr Leu Gln
705 710 715 720
Arg Glu Glu Pro Thr Pro Pro Gly Leu Asp Ser Ser Leu Ser Leu Gly
725 730 735
Ser Gly Met Ser Lys Met Glu Leu Leu Ser Cys Phe Ser Pro Val Leu
740 745 750
Trp Asp Leu Leu Gln Arg Glu Lys Ser Val Trp Ala Leu Arg Thr Leu
755 760 765
Val Lys Ala Tyr Leu Arg Met Pro Pro Glu Asp Leu Gln Gln Leu Val
770 775 780
Leu Ser Ala Glu Met Glu Ala Ala Gln Gly Phe Leu Thr Leu Met Leu
785 790 795 800
Arg Ser Trp Ala Lys Leu Lys Val Gln Pro Ser Glu Glu Gln Ala Met
805 810 815
Gly Arg Leu Thr Ala Leu Leu Leu Gln Arg Tyr Pro Arg Leu Thr Ser
820 825 830
Gln Leu Phe Ile Asp Met Ser Pro Leu Ile Pro Phe Leu Ala Val Pro
835 840 845
Asp Leu Met Arg Phe Pro Pro Ser Leu Leu Ala Asn Asp Ser Val Leu
850 855 860
Ala Ala Ile Arg Asp His Ser Ser Gly Met Lys Pro Glu Gln Lys Glu
865 870 875 880
Ala Leu Ala Lys Arg Leu Leu Ala Pro Glu Leu Phe Gly Glu Val Pro
885 890 895
Asp Trp Pro Gln Glu Leu Leu Trp Ala Ala Leu Pro Leu Leu Pro His
900 905 910
Leu Pro Leu Glu Ser Phe Leu Gln Leu Ser Pro His Gln Ile Gln Ala
915 920 925
Leu Glu Asp Ser Trp Pro Val Ala Asp Leu Gly Pro Gly His Ala Arg
930 935 940
His Val Leu Arg Ser Leu Val Asn Gln Ser Met Glu Asp Gly Glu Glu
945 950 955 960
Gln Val Leu Arg Leu Gly Ser Leu Ala Cys Phe Leu Ser Pro Glu Glu
965 970 975
Leu Gln Ser Leu Val Pro Leu Ser Asp Pro Met Gly Pro Val Glu Gln
980 985 990
Gly Leu Leu Glu Cys Ala Ala Asn Gly Thr Leu Ser Pro Glu Gly Arg
995 1000 1005
Val Ala Tyr Glu Leu Leu Gly Val Leu Arg Ser Ser Gly Gly Thr
1010 1015 1020
Val Leu Ser Pro Arg Glu Leu Arg Val Trp Ala Pro Leu Phe Pro
1025 1030 1035
Gln Leu Gly Leu Arg Phe Leu Gln Glu Leu Ser Glu Thr Gln Leu
1040 1045 1050
Arg Ala Met Leu Pro Ala Leu Gln Gly Ala Ser Val Thr Pro Ala
1055 1060 1065
Gln Ala Val Leu Leu Phe Gly Arg Leu Leu Pro Lys His Asp Leu
1070 1075 1080
Ser Leu Glu Glu Leu Cys Ser Leu His Pro Leu Leu Pro Gly Leu
1085 1090 1095
Ser Pro Gln Thr Leu Gln Ala Ile Pro Lys Arg Val Leu Val Gly
1100 1105 1110
Ala Cys Ser Cys Leu Gly Pro Glu Leu Ser Arg Leu Ser Ala Cys
1115 1120 1125
Gln Ile Ala Ala Leu Leu Gln Thr Phe Arg Val Lys Asp Gly Val
1130 1135 1140
Lys Asn Met Gly Ala Ala Gly Ala Gly Ser Ala Val Cys Ile Pro
1145 1150 1155
Gly Gln Pro Thr Thr Trp Pro Asp Cys Leu Leu Pro Leu Leu Pro
1160 1165 1170
Leu Lys Leu Leu Gln Leu Asp Ala Ala Ala Leu Leu Ala Asn Arg
1175 1180 1185
Arg Leu Tyr Arg Gln Leu Pro Trp Ser Glu Gln Gln Ala Gln Phe
1190 1195 1200
Leu Trp Lys Lys Met Gln Val Pro Thr Asn Leu Ser Leu Arg Asn
1205 1210 1215
Leu Gln Ala Leu Gly Asn Leu Ala Gly Gly Met Thr Cys Glu Phe
1220 1225 1230
Leu Gln Gln Ile Ser Ser Met Val Asp Phe Leu Asp Val Val His
1235 1240 1245
Met Leu Tyr Gln Leu Pro Thr Gly Val Arg Glu Ser Leu Arg Ala
1250 1255 1260
Cys Ile Trp Thr Glu Leu Gln Arg Arg Met Thr Met Pro Glu Pro
1265 1270 1275
Glu Leu Thr Thr Leu Gly Pro Glu Leu Ser Glu Leu Asp Thr Lys
1280 1285 1290
Leu Leu Leu Asp Leu Pro Ile Gln Leu Met Asp Arg Leu Ser Asn
1295 1300 1305
Asp Ser Ile Met Leu Val Val Glu Met Val Gln Gly Ala Pro Glu
1310 1315 1320
Gln Leu Leu Ala Leu Thr Pro Leu His Gln Thr Ala Leu Ala Glu
1325 1330 1335
Arg Ala Leu Lys Asn Leu Ala Pro Lys Glu Thr Pro Ile Ser Lys
1340 1345 1350
Glu Val Leu Glu Thr Leu Gly Pro Leu Val Gly Phe Leu Gly Ile
1355 1360 1365
Glu Ser Thr Arg Arg Ile Pro Leu Pro Ile Leu Leu Ser His Leu
1370 1375 1380
Ser Gln Leu Gln Gly Phe Cys Leu Gly Glu Thr Phe Ala Thr Glu
1385 1390 1395
Leu Gly Trp Leu Leu Leu Gln Glu Pro Val Leu Gly Lys Pro Glu
1400 1405 1410
Leu Trp Ser Gln Asp Glu Ile Glu Gln Ala Gly Arg Leu Val Phe
1415 1420 1425
Thr Leu Ser Ala Glu Ala Ile Ser Ser Ile Pro Arg Glu Ala Leu
1430 1435 1440
Gly Pro Glu Thr Leu Glu Arg Leu Leu Gly Lys His Gln Ser Trp
1445 1450 1455
Glu Gln Ser Arg Val Gly His Leu Cys Gly Glu Ser Gln Leu Ala
1460 1465 1470
His Lys Lys Ala Ala Leu Val Ala Gly Ile Val His Pro Ala Ala
1475 1480 1485
Glu Gly Leu Gln Glu Pro Val Pro Asn Cys Ala Asp Ile Arg Gly
1490 1495 1500
Thr Phe Pro Ala Ala Trp Ser Ala Thr Gln Ile Ser Glu Met Glu
1505 1510 1515
Leu Ser Asp Phe Glu Asp Cys Leu Ser Leu Phe Ala Gly Asp Pro
1520 1525 1530
Gly Leu Gly Pro Glu Glu Leu Arg Ala Ala Met Gly Lys Ala Lys
1535 1540 1545
Gln Leu Trp Gly Pro Pro Arg Gly Phe Arg Pro Glu Gln Ile Leu
1550 1555 1560
Gln Leu Gly Arg Leu Leu Ile Gly Leu Gly Glu Arg Glu Leu Gln
1565 1570 1575
Glu Leu Thr Leu Val Asp Trp Gly Val Leu Ser Ser Leu Gly Gln
1580 1585 1590
Ile Asp Gly Trp Ser Ser Met Gln Leu Arg Ala Val Val Ser Ser
1595 1600 1605
Phe Leu Arg Gln Ser Gly Arg His Val Ser His Leu Asp Phe Ile
1610 1615 1620
Tyr Leu Thr Ala Leu Gly Tyr Thr Val Cys Gly Leu Arg Pro Glu
1625 1630 1635
Glu Leu Gln His Ile Ser Ser Trp Glu Phe Ser Gln Ala Ala Leu
1640 1645 1650
Phe Leu Gly Ser Leu His Leu Pro Cys Ser Glu Glu Gln Leu Glu
1655 1660 1665
Val Leu Ala Tyr Leu Leu Val Leu Pro Gly Gly Phe Gly Pro Val
1670 1675 1680
Ser Asn Trp Gly Pro Glu Ile Phe Thr Glu Ile Gly Thr Ile Ala
1685 1690 1695
Ala Gly Ile Pro Asp Leu Ala Leu Ser Ala Leu Leu Arg Gly Gln
1700 1705 1710
Ile Gln Gly Leu Thr Pro Leu Ala Ile Ser Val Ile Pro Ala Pro
1715 1720 1725
Lys Phe Ala Val Val Phe Asn Pro Ile Gln Leu Ser Ser Leu Thr
1730 1735 1740
Arg Gly Gln Ala Val Ala Val Thr Pro Glu Gln Leu Ala Tyr Leu
1745 1750 1755
Ser Pro Glu Gln Arg Arg Ala Val Ala Trp Ala Gln His Glu Gly
1760 1765 1770
Lys Glu Ile Pro Glu Gln Leu Gly Arg Asn Ser Ala Trp Gly Leu
1775 1780 1785
Tyr Asp Trp Phe Gln Ala Ser Trp Ala Leu Ala Leu Pro Val Ser
1790 1795 1800
Ile Phe Gly His Leu Leu Thr Arg Thr Arg Pro Leu Glu Gln Lys
1805 1810 1815
Leu Ile Ser Glu Glu Asp Leu
1820 1825
<210> 40
<211> 60
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
oligonucleotide
<400> 40
gctctcagcc tctggcccct gctgctgctg ctgctgctgc tgctgctgct gtcctttgca 60
<210> 41
<211> 63
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
oligonucleotide
<400> 41
gctctgagcc tccagcccca gctgctcctt ctcctgtcgc tcctgccgca ggaagtgact 60
tca 63
<210> 42
<211> 312
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 42
tgcctgtcat acgaaaccga gatactgaca gtagaatatg gccttctgcc aatcgggaag 60
attgtggaga aacggataga atgcacagtt tactctgtcg ataacaatgg taacatttat 120
actcagccag ttgcccagtg gcacgaccgg ggagagcagg aagtattcga atactgtctg 180
gaggatggaa gtctcattag ggccactaag gaccacaaat ttatgacagt cgatggccag 240
atgctgccta tagacgaaat ctttgagcga gagttggacc tcatgcgagt tgacaacctt 300
cctaattaat ag 312
<210> 43
<211> 20
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 43
Ala Leu Ser Leu Trp Pro Leu Leu Leu Leu Leu Leu Leu Leu Leu Leu
1 5 10 15
Leu Ser Phe Ala
20
<210> 44
<211> 21
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 44
Ala Leu Ser Leu Gln Pro Gln Leu Leu Leu Leu Leu Ser Leu Leu Pro
1 5 10 15
Gln Glu Val Thr Ser
20
<210> 45
<211> 102
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 45
Cys Leu Ser Tyr Glu Thr Glu Ile Leu Thr Val Glu Tyr Gly Leu Leu
1 5 10 15
Pro Ile Gly Lys Ile Val Glu Lys Arg Ile Glu Cys Thr Val Tyr Ser
20 25 30
Val Asp Asn Asn Gly Asn Ile Tyr Thr Gln Pro Val Ala Gln Trp His
35 40 45
Asp Arg Gly Glu Gln Glu Val Phe Glu Tyr Cys Leu Glu Asp Gly Ser
50 55 60
Leu Ile Arg Ala Thr Lys Asp His Lys Phe Met Thr Val Asp Gly Gln
65 70 75 80
Met Leu Pro Ile Asp Glu Ile Phe Glu Arg Glu Leu Asp Leu Met Arg
85 90 95
Val Asp Asn Leu Pro Asn
100
<210> 46
<211> 105
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 46
atcaagatag ctacaaggaa gtatcttggc aaacaaaacg tttatgatat tggagtcgaa 60
agagatcaca actttgctct gaagaacgga ttcatagctt ctaat 105
<210> 47
<211> 18
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
oligonucleotide
<400> 47
acgcgtacgc ggccgctc 18
<210> 48
<211> 36
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
oligonucleotide
<400> 48
gagcagaaac tcatctcaga agaggatctg taatag 36
<210> 49
<211> 35
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 49
Ile Lys Ile Ala Thr Arg Lys Tyr Leu Gly Lys Gln Asn Val Tyr Asp
1 5 10 15
Ile Gly Val Glu Arg Asp His Asn Phe Ala Leu Lys Asn Gly Phe Ile
20 25 30
Ala Ser Asn
35
<210> 50
<211> 6
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 50
Thr Arg Thr Arg Pro Leu
1 5
<210> 51
<211> 3219
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 51
atggctctga gcctccagcc ccagctgctc cttctcctgt cgctcctgcc gcaggaagtg 60
acttcagccc ctactgggcc tcagtctttg gatgctggtc tctcccttct gaagtcattc 120
gtagccactc tggaccaagc tcctcagcgt tccctcagcc agtcacggtt ctctgcgttc 180
ctggccaaca tttcttcatc cttccagctt gggaggatgg gggagggacc ggtgggagag 240
cccccacctc tccagccccc tgcacttcga cttcatgatt tcctcgtgac actgagaggt 300
agcccagact gggagccaat gctagggctt ctgggagatg tgctggcact cctgggacag 360
gaacagactc cccgggactt tttggtgcac caggcaggtg tactgggtgg acttgtagag 420
gcattgttgg gagcgttagt tcctggaggc ccccctgccc ccactcgacc cccatgcacc 480
cgtgatggcc cttctgactg tgtcctggct gctgattggt tgccttctct gatgttgtta 540
ttagagggta cacgctggca ggccctggtg cagttgcagc ccagtgtgga cccaaccaat 600
gccacaggtc ttgatggtag agagccagct cctcactttt tacagggtct gctgggcttg 660
cttaccccag caggagagtt gggctctgag gaggctcttt ggggtggtct gctgcgcaca 720
gtgggggccc ccctctatgc tgccttccag gaggggctac tgcgagtcac tcattctctg 780
caagatgagg tcttttctat tatgggacag ccagagcctg atgccagtgg gcagtgccag 840
ggaggcaacc ttcaacagct gcttttatgg ggcatgcgga acaacctttc ttgggacgcc 900
cgagcactgg gttttctatc tggatcacca cctccacccc ctgctctcct gcactgcctg 960
agcagaggtg tgcctctgcc cagggcttcc cagcctgcgg ctcacatcag ccctcgacag 1020
cggcgagcca tctctgtgga ggccctctgc gagaaccact caggcccaga gccaccctac 1080
agcatctcca acttctccat ctacttgctc tgccagcaca tcaagcctgc caccccgcgg 1140
ccccctccta ccaccccacg gcctcctcct accaccccac agccccctcc taccactaca 1200
cagcccattc ctgacactac acagccccct cctgtcaccc caaggcctcc tcctaccacc 1260
ccacaacccc ctcctagcac agctgtcatc tgccagacag ctgtatggta cgcagtctcg 1320
tgggcaccag gtgcccgagg ttggctccaa gcctgccatg atcagtttcc tgatcaattt 1380
ctggatatga tctgcggcaa cctctcattt tcagccctgt ctggccccag tcgtcctttg 1440
gtaaagcagc tctgtgctgg cttgctccca ccccccacta gctgtccacc aggcctgatc 1500
cctgtgcccc tcaccccaga aatattctgg ggctgtttcc tggagaatga gacactgtgg 1560
gctgaacggt tgtgtgtgga ggacagtctg caggctgtgc ccccgaggaa ccaggcttgg 1620
gttcagcatg tgtgtcgggg ccccaccttg gacgccactg attttccacc gtgccgcgtt 1680
ggaccctgtg gggaacgctg cccagatggg ggcagcttcc tgctcatggt ctgtgccaat 1740
gacactctgt atgaagcctt ggttcccttc tgggcttggc tagcaggcca atgcagaatt 1800
agtcgtggag gaaatgatac ttgctttcta gaaggcatgc tgggcccctt gttgccctct 1860
ctgccccctc tgggaccatc cccactctgt ctggctcctg gtccttttct gcttggcatg 1920
ttatcccagt tgccacgctg tcagtcctcc gtgccagccc tcgcccaccc cacgcgccta 1980
cattacctcc tgcgcctact gaccttcctt ctgggtccag ggactggggg tgccgagacg 2040
caggggatgt taggtcaagc cctgctgctc tctagtctcc cagacaactg ttcattctgg 2100
gatgccttcc gcccagaggg ccggagaagt gtactgagga cagtcggaga gtacttgcag 2160
cgggaagagc caaccccacc aggcttagac tcctccctca gcctcggctc tggtatgagc 2220
aagatggagc ttctgtcctg cttcagtcct gtactgtggg atctactcca gagagagaag 2280
agcgtttggg ccctgaggac cctggtgaag gcctacctgc gcatgcctcc agaagacctt 2340
cagcagcttg tgctttcagc agagatggag gctgcacagg gcttcctgac gctcatgctt 2400
cgttcctggg ctaagctgaa ggttcaacca tccgaggagc aggccatggg ccgcctgaca 2460
gccttgctgc tccagcggta cccacgcctc acctcccaac tctttatcga catgtcaccg 2520
ctcatcccct tcctggctgt ccctgacctc atgcgcttcc caccgtccct tttggccaac 2580
gacagtgtcc tggctgccat cagggatcac agctcaggaa tgaagcctga acagaaggag 2640
gccctggcaa aacgactgct ggcccctgag ctgtttggag aagtgcctga ttggccccag 2700
gagctgctgt gggcagccct gcctctgctt ccccatctgc ctctggagag ctttctccag 2760
ctcagccctc accagatcca ggccctggag gatagctggc cagtagcaga tcttgggccg 2820
ggacacgccc gacatgtgct tcgtagccta gtaaaccaga gcatggagga tggggaggag 2880
caggtgctca ggcttgggtc cctcgcctgc ctgtcatacg aaaccgagat actgacagta 2940
gaatatggcc ttctgccaat cgggaagatt gtggagaaac ggatagaatg cacagtttac 3000
tctgtcgata acaatggtaa catttatact cagccagttg cccagtggca cgaccgggga 3060
gagcaggaag tattcgaata ctgtctggag gatggaagtc tcattagggc cactaaggac 3120
cacaaattta tgacagtcga tggccagatg ctgcctatag acgaaatctt tgagcgagag 3180
ttggacctca tgcgagttga caaccttcct aattaatag 3219
<210> 52
<211> 1071
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 52
Met Ala Leu Ser Leu Gln Pro Gln Leu Leu Leu Leu Leu Ser Leu Leu
1 5 10 15
Pro Gln Glu Val Thr Ser Ala Pro Thr Gly Pro Gln Ser Leu Asp Ala
20 25 30
Gly Leu Ser Leu Leu Lys Ser Phe Val Ala Thr Leu Asp Gln Ala Pro
35 40 45
Gln Arg Ser Leu Ser Gln Ser Arg Phe Ser Ala Phe Leu Ala Asn Ile
50 55 60
Ser Ser Ser Phe Gln Leu Gly Arg Met Gly Glu Gly Pro Val Gly Glu
65 70 75 80
Pro Pro Pro Leu Gln Pro Pro Ala Leu Arg Leu His Asp Phe Leu Val
85 90 95
Thr Leu Arg Gly Ser Pro Asp Trp Glu Pro Met Leu Gly Leu Leu Gly
100 105 110
Asp Val Leu Ala Leu Leu Gly Gln Glu Gln Thr Pro Arg Asp Phe Leu
115 120 125
Val His Gln Ala Gly Val Leu Gly Gly Leu Val Glu Ala Leu Leu Gly
130 135 140
Ala Leu Val Pro Gly Gly Pro Pro Ala Pro Thr Arg Pro Pro Cys Thr
145 150 155 160
Arg Asp Gly Pro Ser Asp Cys Val Leu Ala Ala Asp Trp Leu Pro Ser
165 170 175
Leu Met Leu Leu Leu Glu Gly Thr Arg Trp Gln Ala Leu Val Gln Leu
180 185 190
Gln Pro Ser Val Asp Pro Thr Asn Ala Thr Gly Leu Asp Gly Arg Glu
195 200 205
Pro Ala Pro His Phe Leu Gln Gly Leu Leu Gly Leu Leu Thr Pro Ala
210 215 220
Gly Glu Leu Gly Ser Glu Glu Ala Leu Trp Gly Gly Leu Leu Arg Thr
225 230 235 240
Val Gly Ala Pro Leu Tyr Ala Ala Phe Gln Glu Gly Leu Leu Arg Val
245 250 255
Thr His Ser Leu Gln Asp Glu Val Phe Ser Ile Met Gly Gln Pro Glu
260 265 270
Pro Asp Ala Ser Gly Gln Cys Gln Gly Gly Asn Leu Gln Gln Leu Leu
275 280 285
Leu Trp Gly Met Arg Asn Asn Leu Ser Trp Asp Ala Arg Ala Leu Gly
290 295 300
Phe Leu Ser Gly Ser Pro Pro Pro Pro Pro Ala Leu Leu His Cys Leu
305 310 315 320
Ser Arg Gly Val Pro Leu Pro Arg Ala Ser Gln Pro Ala Ala His Ile
325 330 335
Ser Pro Arg Gln Arg Arg Ala Ile Ser Val Glu Ala Leu Cys Glu Asn
340 345 350
His Ser Gly Pro Glu Pro Pro Tyr Ser Ile Ser Asn Phe Ser Ile Tyr
355 360 365
Leu Leu Cys Gln His Ile Lys Pro Ala Thr Pro Arg Pro Pro Pro Thr
370 375 380
Thr Pro Arg Pro Pro Pro Thr Thr Pro Gln Pro Pro Pro Thr Thr Thr
385 390 395 400
Gln Pro Ile Pro Asp Thr Thr Gln Pro Pro Pro Val Thr Pro Arg Pro
405 410 415
Pro Pro Thr Thr Pro Gln Pro Pro Pro Ser Thr Ala Val Ile Cys Gln
420 425 430
Thr Ala Val Trp Tyr Ala Val Ser Trp Ala Pro Gly Ala Arg Gly Trp
435 440 445
Leu Gln Ala Cys His Asp Gln Phe Pro Asp Gln Phe Leu Asp Met Ile
450 455 460
Cys Gly Asn Leu Ser Phe Ser Ala Leu Ser Gly Pro Ser Arg Pro Leu
465 470 475 480
Val Lys Gln Leu Cys Ala Gly Leu Leu Pro Pro Pro Thr Ser Cys Pro
485 490 495
Pro Gly Leu Ile Pro Val Pro Leu Thr Pro Glu Ile Phe Trp Gly Cys
500 505 510
Phe Leu Glu Asn Glu Thr Leu Trp Ala Glu Arg Leu Cys Val Glu Asp
515 520 525
Ser Leu Gln Ala Val Pro Pro Arg Asn Gln Ala Trp Val Gln His Val
530 535 540
Cys Arg Gly Pro Thr Leu Asp Ala Thr Asp Phe Pro Pro Cys Arg Val
545 550 555 560
Gly Pro Cys Gly Glu Arg Cys Pro Asp Gly Gly Ser Phe Leu Leu Met
565 570 575
Val Cys Ala Asn Asp Thr Leu Tyr Glu Ala Leu Val Pro Phe Trp Ala
580 585 590
Trp Leu Ala Gly Gln Cys Arg Ile Ser Arg Gly Gly Asn Asp Thr Cys
595 600 605
Phe Leu Glu Gly Met Leu Gly Pro Leu Leu Pro Ser Leu Pro Pro Leu
610 615 620
Gly Pro Ser Pro Leu Cys Leu Ala Pro Gly Pro Phe Leu Leu Gly Met
625 630 635 640
Leu Ser Gln Leu Pro Arg Cys Gln Ser Ser Val Pro Ala Leu Ala His
645 650 655
Pro Thr Arg Leu His Tyr Leu Leu Arg Leu Leu Thr Phe Leu Leu Gly
660 665 670
Pro Gly Thr Gly Gly Ala Glu Thr Gln Gly Met Leu Gly Gln Ala Leu
675 680 685
Leu Leu Ser Ser Leu Pro Asp Asn Cys Ser Phe Trp Asp Ala Phe Arg
690 695 700
Pro Glu Gly Arg Arg Ser Val Leu Arg Thr Val Gly Glu Tyr Leu Gln
705 710 715 720
Arg Glu Glu Pro Thr Pro Pro Gly Leu Asp Ser Ser Leu Ser Leu Gly
725 730 735
Ser Gly Met Ser Lys Met Glu Leu Leu Ser Cys Phe Ser Pro Val Leu
740 745 750
Trp Asp Leu Leu Gln Arg Glu Lys Ser Val Trp Ala Leu Arg Thr Leu
755 760 765
Val Lys Ala Tyr Leu Arg Met Pro Pro Glu Asp Leu Gln Gln Leu Val
770 775 780
Leu Ser Ala Glu Met Glu Ala Ala Gln Gly Phe Leu Thr Leu Met Leu
785 790 795 800
Arg Ser Trp Ala Lys Leu Lys Val Gln Pro Ser Glu Glu Gln Ala Met
805 810 815
Gly Arg Leu Thr Ala Leu Leu Leu Gln Arg Tyr Pro Arg Leu Thr Ser
820 825 830
Gln Leu Phe Ile Asp Met Ser Pro Leu Ile Pro Phe Leu Ala Val Pro
835 840 845
Asp Leu Met Arg Phe Pro Pro Ser Leu Leu Ala Asn Asp Ser Val Leu
850 855 860
Ala Ala Ile Arg Asp His Ser Ser Gly Met Lys Pro Glu Gln Lys Glu
865 870 875 880
Ala Leu Ala Lys Arg Leu Leu Ala Pro Glu Leu Phe Gly Glu Val Pro
885 890 895
Asp Trp Pro Gln Glu Leu Leu Trp Ala Ala Leu Pro Leu Leu Pro His
900 905 910
Leu Pro Leu Glu Ser Phe Leu Gln Leu Ser Pro His Gln Ile Gln Ala
915 920 925
Leu Glu Asp Ser Trp Pro Val Ala Asp Leu Gly Pro Gly His Ala Arg
930 935 940
His Val Leu Arg Ser Leu Val Asn Gln Ser Met Glu Asp Gly Glu Glu
945 950 955 960
Gln Val Leu Arg Leu Gly Ser Leu Ala Cys Leu Ser Tyr Glu Thr Glu
965 970 975
Ile Leu Thr Val Glu Tyr Gly Leu Leu Pro Ile Gly Lys Ile Val Glu
980 985 990
Lys Arg Ile Glu Cys Thr Val Tyr Ser Val Asp Asn Asn Gly Asn Ile
995 1000 1005
Tyr Thr Gln Pro Val Ala Gln Trp His Asp Arg Gly Glu Gln Glu
1010 1015 1020
Val Phe Glu Tyr Cys Leu Glu Asp Gly Ser Leu Ile Arg Ala Thr
1025 1030 1035
Lys Asp His Lys Phe Met Thr Val Asp Gly Gln Met Leu Pro Ile
1040 1045 1050
Asp Glu Ile Phe Glu Arg Glu Leu Asp Leu Met Arg Val Asp Asn
1055 1060 1065
Leu Pro Asn
1070
<210> 53
<211> 2745
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 53
atggctctga gcctccagcc ccagctgctc cttctcctgt cgctcctgcc gcaggaagtg 60
acttcaatca agatagctac aaggaagtat cttggcaaac aaaacgttta tgatattgga 120
gtcgaaagag atcacaactt tgctctgaag aacggattca tagcttctaa ttgtttcctg 180
agtcctgagg agctacagag tctggtgccc ttgagtgatc caatggggcc tgtagaacag 240
ggtctgctgg aatgtgcggc caatgggacc ctcagcccag aaggacgggt ggcatatgaa 300
cttctgggag tgttgcgttc atctggagga actgtcttaa gcccccgaga gctgagggtc 360
tgggcacctc tctttcccca gctgggcctc cgcttcctgc aggagctctc agagacccag 420
cttagagcca tgcttcctgc cctacaggga gccagtgtca cacctgccca ggctgttctg 480
ttgtttggaa ggctccttcc taagcatgat ctgtccctgg aggaactctg ctccctgcac 540
cctctcctgc caggtctcag cccccagaca ctccaggcca tccctaagag agttctggtt 600
ggtgcttgtt cctgcctggg ccctgaactg tcaaggcttt cagcttgcca gattgcagct 660
ctgctgcaga cctttcgggt aaaagatggt gttaaaaata tgggtgcagc aggtgccggc 720
tcagccgtgt gcattcctgg gcagcccacc acttggccag actgcctgct tcccctgctc 780
ccattaaagc tgctacagct ggacgctgca gctcttctgg caaaccgaag actctatcgg 840
cagctgcctt ggtctgagca acaggcacag tttctctgga agaaaatgca agtgcctacc 900
aacctgagcc tgaggaatct gcaggctctg ggcaacttgg caggaggcat gacctgcgag 960
tttctgcagc agatcagctc aatggttgac tttcttgatg tggtacacat gctctaccag 1020
ctgcccactg gtgttcgaga gagcctgcgg gcctgtatct ggacagagct acagcggagg 1080
atgacaatgc cagagccaga gctgaccacc ctagggccag aactgagtga acttgacaca 1140
aagctactcc tggacttgcc gatccagctg atggacagat tgtccaatga ttccattatg 1200
ttggtggtgg agatggtcca aggcgctcca gagcagctgc tggcactgac cccactccac 1260
cagacagcct tggcagagcg agcacttaaa aacctggctc caaaggagac cccaatctcc 1320
aaagaagtgc tggagacact gggccccttg gttggattcc tgggaataga gagcacgcga 1380
cggatccctt tacccattct actgtctcat ctcagtcagc tgcagggctt ctgcctagga 1440
gagacatttg ccacagagct gggatggctg ctgttgcagg agcctgttct tggaaaacca 1500
gaattgtgga gccaggatga aatagagcaa gctggacgcc tagtattcac tctgtctgct 1560
gaggctattt cctcgatccc cagggaggct ttgggcccag agacactgga gaggcttctg 1620
ggaaagcatc aaagctggga gcagagcaga gtgggccatc tgtgtgggga gtcacagctt 1680
gcccacaaga aagcagctct ggtagctggg attgtgcatc cagctgctga gggtctccaa 1740
gagcctgtac caaactgtgc agacatacgg ggaaccttcc cagcggcctg gtctgcgaca 1800
caaatctcag agatggaact ctcagacttt gaagactgcc tgtcactatt tgctggagat 1860
ccaggacttg gtcctgagga actacgggca gccatgggca aggccaagca gttgtggggt 1920
ccccctcgag gattccgtcc tgagcagatc ttgcagctgg gccgtctcct gataggtcta 1980
ggagaacggg aactgcagga gcttaccttg gtggactggg gtgtgctgag cagcctgggg 2040
caaatagatg gctggagttc catgcagctc cgagccgtgg tctccagttt cctaaggcag 2100
agtggtcggc atgtgagcca cctggacttc atttatctga cagcactggg ttacacagtc 2160
tgtggattgc gaccagagga gttacagcac atcagcagtt gggagtttag ccaagcagct 2220
ctcttcctgg gtagcttgca tctcccgtgc tctgaggaac agctggaagt tctggcctat 2280
ctccttgtgt tgcctggtgg ctttggccca gtcagtaact gggggcctga gatcttcact 2340
gaaattggca caatagcagc tggcatccca gacctggctc tttcagcatt actgcgggga 2400
cagatccaag gcctgactcc tcttgccatt tctgtcattc ctgctcccaa gtttgcagtg 2460
gtcttcaacc ccatccagtt atctagtctc accaggggtc aggccgtagc tgttactcct 2520
gaacagctgg cctatctgag tcctgagcag cggcgagcag ttgcatgggc ccaacacgaa 2580
gggaaggaga tcccagagca gctgggtcga aactcagcct ggggtctcta cgactggttc 2640
caagcctcct gggccctggc attgcccgtc agcatttttg gccacctatt aacgcgtacg 2700
cggccgctcg agcagaaact catctcagaa gaggatctgt aatag 2745
<210> 54
<211> 913
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polypeptide
<400> 54
Met Ala Leu Ser Leu Gln Pro Gln Leu Leu Leu Leu Leu Ser Leu Leu
1 5 10 15
Pro Gln Glu Val Thr Ser Ile Lys Ile Ala Thr Arg Lys Tyr Leu Gly
20 25 30
Lys Gln Asn Val Tyr Asp Ile Gly Val Glu Arg Asp His Asn Phe Ala
35 40 45
Leu Lys Asn Gly Phe Ile Ala Ser Asn Cys Phe Leu Ser Pro Glu Glu
50 55 60
Leu Gln Ser Leu Val Pro Leu Ser Asp Pro Met Gly Pro Val Glu Gln
65 70 75 80
Gly Leu Leu Glu Cys Ala Ala Asn Gly Thr Leu Ser Pro Glu Gly Arg
85 90 95
Val Ala Tyr Glu Leu Leu Gly Val Leu Arg Ser Ser Gly Gly Thr Val
100 105 110
Leu Ser Pro Arg Glu Leu Arg Val Trp Ala Pro Leu Phe Pro Gln Leu
115 120 125
Gly Leu Arg Phe Leu Gln Glu Leu Ser Glu Thr Gln Leu Arg Ala Met
130 135 140
Leu Pro Ala Leu Gln Gly Ala Ser Val Thr Pro Ala Gln Ala Val Leu
145 150 155 160
Leu Phe Gly Arg Leu Leu Pro Lys His Asp Leu Ser Leu Glu Glu Leu
165 170 175
Cys Ser Leu His Pro Leu Leu Pro Gly Leu Ser Pro Gln Thr Leu Gln
180 185 190
Ala Ile Pro Lys Arg Val Leu Val Gly Ala Cys Ser Cys Leu Gly Pro
195 200 205
Glu Leu Ser Arg Leu Ser Ala Cys Gln Ile Ala Ala Leu Leu Gln Thr
210 215 220
Phe Arg Val Lys Asp Gly Val Lys Asn Met Gly Ala Ala Gly Ala Gly
225 230 235 240
Ser Ala Val Cys Ile Pro Gly Gln Pro Thr Thr Trp Pro Asp Cys Leu
245 250 255
Leu Pro Leu Leu Pro Leu Lys Leu Leu Gln Leu Asp Ala Ala Ala Leu
260 265 270
Leu Ala Asn Arg Arg Leu Tyr Arg Gln Leu Pro Trp Ser Glu Gln Gln
275 280 285
Ala Gln Phe Leu Trp Lys Lys Met Gln Val Pro Thr Asn Leu Ser Leu
290 295 300
Arg Asn Leu Gln Ala Leu Gly Asn Leu Ala Gly Gly Met Thr Cys Glu
305 310 315 320
Phe Leu Gln Gln Ile Ser Ser Met Val Asp Phe Leu Asp Val Val His
325 330 335
Met Leu Tyr Gln Leu Pro Thr Gly Val Arg Glu Ser Leu Arg Ala Cys
340 345 350
Ile Trp Thr Glu Leu Gln Arg Arg Met Thr Met Pro Glu Pro Glu Leu
355 360 365
Thr Thr Leu Gly Pro Glu Leu Ser Glu Leu Asp Thr Lys Leu Leu Leu
370 375 380
Asp Leu Pro Ile Gln Leu Met Asp Arg Leu Ser Asn Asp Ser Ile Met
385 390 395 400
Leu Val Val Glu Met Val Gln Gly Ala Pro Glu Gln Leu Leu Ala Leu
405 410 415
Thr Pro Leu His Gln Thr Ala Leu Ala Glu Arg Ala Leu Lys Asn Leu
420 425 430
Ala Pro Lys Glu Thr Pro Ile Ser Lys Glu Val Leu Glu Thr Leu Gly
435 440 445
Pro Leu Val Gly Phe Leu Gly Ile Glu Ser Thr Arg Arg Ile Pro Leu
450 455 460
Pro Ile Leu Leu Ser His Leu Ser Gln Leu Gln Gly Phe Cys Leu Gly
465 470 475 480
Glu Thr Phe Ala Thr Glu Leu Gly Trp Leu Leu Leu Gln Glu Pro Val
485 490 495
Leu Gly Lys Pro Glu Leu Trp Ser Gln Asp Glu Ile Glu Gln Ala Gly
500 505 510
Arg Leu Val Phe Thr Leu Ser Ala Glu Ala Ile Ser Ser Ile Pro Arg
515 520 525
Glu Ala Leu Gly Pro Glu Thr Leu Glu Arg Leu Leu Gly Lys His Gln
530 535 540
Ser Trp Glu Gln Ser Arg Val Gly His Leu Cys Gly Glu Ser Gln Leu
545 550 555 560
Ala His Lys Lys Ala Ala Leu Val Ala Gly Ile Val His Pro Ala Ala
565 570 575
Glu Gly Leu Gln Glu Pro Val Pro Asn Cys Ala Asp Ile Arg Gly Thr
580 585 590
Phe Pro Ala Ala Trp Ser Ala Thr Gln Ile Ser Glu Met Glu Leu Ser
595 600 605
Asp Phe Glu Asp Cys Leu Ser Leu Phe Ala Gly Asp Pro Gly Leu Gly
610 615 620
Pro Glu Glu Leu Arg Ala Ala Met Gly Lys Ala Lys Gln Leu Trp Gly
625 630 635 640
Pro Pro Arg Gly Phe Arg Pro Glu Gln Ile Leu Gln Leu Gly Arg Leu
645 650 655
Leu Ile Gly Leu Gly Glu Arg Glu Leu Gln Glu Leu Thr Leu Val Asp
660 665 670
Trp Gly Val Leu Ser Ser Leu Gly Gln Ile Asp Gly Trp Ser Ser Met
675 680 685
Gln Leu Arg Ala Val Val Ser Ser Phe Leu Arg Gln Ser Gly Arg His
690 695 700
Val Ser His Leu Asp Phe Ile Tyr Leu Thr Ala Leu Gly Tyr Thr Val
705 710 715 720
Cys Gly Leu Arg Pro Glu Glu Leu Gln His Ile Ser Ser Trp Glu Phe
725 730 735
Ser Gln Ala Ala Leu Phe Leu Gly Ser Leu His Leu Pro Cys Ser Glu
740 745 750
Glu Gln Leu Glu Val Leu Ala Tyr Leu Leu Val Leu Pro Gly Gly Phe
755 760 765
Gly Pro Val Ser Asn Trp Gly Pro Glu Ile Phe Thr Glu Ile Gly Thr
770 775 780
Ile Ala Ala Gly Ile Pro Asp Leu Ala Leu Ser Ala Leu Leu Arg Gly
785 790 795 800
Gln Ile Gln Gly Leu Thr Pro Leu Ala Ile Ser Val Ile Pro Ala Pro
805 810 815
Lys Phe Ala Val Val Phe Asn Pro Ile Gln Leu Ser Ser Leu Thr Arg
820 825 830
Gly Gln Ala Val Ala Val Thr Pro Glu Gln Leu Ala Tyr Leu Ser Pro
835 840 845
Glu Gln Arg Arg Ala Val Ala Trp Ala Gln His Glu Gly Lys Glu Ile
850 855 860
Pro Glu Gln Leu Gly Arg Asn Ser Ala Trp Gly Leu Tyr Asp Trp Phe
865 870 875 880
Gln Ala Ser Trp Ala Leu Ala Leu Pro Val Ser Ile Phe Gly His Leu
885 890 895
Leu Thr Arg Thr Arg Pro Leu Glu Gln Lys Leu Ile Ser Glu Glu Asp
900 905 910
Leu
<210> 55
<211> 2124
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 55
atggctctca gcctctggcc cctgctgctg ctgctgctgc tgctgctgct gctgtccttt 60
gcagtgactc tggcccctac tgggcctcat tccctggacc ctggtctctc cttcctgaag 120
tcattgctct ccactctgga ccaggctccc cagggctccc tgagccgctc acggttcttt 180
acattcctgg ccaacatttc ttcttccttt gagcctggga gaatggggga aggaccagta 240
ggagagcccc cacctctcca gccgcctgct ctgcggctcc atgattttct agtgacactg 300
agaggtagcc ccgactggga gccaatgcta gggctgctag gggatatgct ggcactgctg 360
ggacaggagc agactccccg agatttcctg gtgcaccagg caggggtgct gggtggactt 420
gtggaggtgc tgctgggagc cttagttcct gggggccccc ctaccccaac tcggccccca 480
tgcacccgtg atgggccgtc tgactgtgtc ctggctgctg actggttgcc ttctctgctg 540
ctgttgttag agggcacacg ctggcaagct ctggtgcagg tgcagcccag tgtggacccc 600
accaatgcca caggcctcga tgggagggag gcagctcctc actttttgca gggtctgttg 660
ggtttgctta ccccaacagg ggagctaggc tccaaggagg ctctttgggg cggtctgcta 720
cgcacagtgg gggcccccct ctatgctgcc tttcaggagg ggctgctccg tgtcactcac 780
tccctgcagg atgaggtctt ctccattttg gggcagccag agcctgatac caatgggcag 840
tgccagggag gtaaccttca acagctgctc ttatggggcg tccggcacaa cctttcctgg 900
gatgtccagg cgctgggctt tctgtctgga tcaccacccc caccccctgc cctccttcac 960
tgcctgagca cgggcgtgcc tctgcccaga gcttctcagc cgtcagccca catcagccca 1020
cgccaacggc gagccatcac tgtggaggcc ctctgtgaga accacttagg cccagcacca 1080
ccctacagca tttccaactt ctccatccac ttgctctgcc agcacaccaa gcctgccact 1140
ccacagcccc atcccagcac cactgccatc tgccagacag ctgtgtggta tgcagtgtcc 1200
tgggcaccag gtgcccaagg ctggctacag gcctgccacg accagtttcc tgatgagttt 1260
ttggatgcga tctgcagtaa cctctccttt tcagccctgt ctggctccaa ccgccgcctg 1320
gtgaagcggc tctgtgctgg cctgctccca ccccctacca gctgccctga aggcctgccc 1380
cctgttcccc tcaccccaga catcttttgg ggctgcttct tggagaatga gactctgtgg 1440
gctgagcgac tgtgtgggga ggcaagtcta caggctgtgc cccccagcaa ccaggcttgg 1500
gtccagcatg tgtgccaggg ccccacccca gatgtcactg cctccccacc atgccacatt 1560
ggaccctgtg gggaacgctg cccggatggg ggcagcttcc tggtgatggt ctgtgccaat 1620
gacaccatgt atgaggtcct ggtgcccttc tggccttggc tagcaggcca atgcaggata 1680
agtcgtgggg gcaatgacac ttgcttccta gaagggctgc tgggccccct tctgccctct 1740
ctgccaccac tgggaccatc cccactctgt ctgacccctg gccccttcct ccttggcatg 1800
ctatcccagt tgccacgctg tcagtcctct gtcccagctc ttgctcaccc cacacgccta 1860
cactatctcc tccgcctgct gaccttcctc ttgggtccag gggctggggg cgctgaggcc 1920
caggggatgc tgggtcgggc cctactgctc tccagtctcc cagacaactg ctccttctgg 1980
gatgcctttc gcccagaggg ccggcgcagt gtgctacgga cgattgggga atacctggaa 2040
caagatgagg agcagccaac cccatcaggc tttgaaccca ctgtcaaccc cagctctggt 2100
ataagcaaga tggagctgct ggcc 2124
<210> 56
<211> 2238
<212> DNA
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
polynucleotide
<400> 56
atggctctga gcctccagcc ccagctgctc cttctcctgt cgctcctgcc gcaggaagtg 60
acttcagccc ctactgggcc tcagtctttg gatgctggtc tctcccttct gaagtcattc 120
gtagccactc tggaccaagc tcctcagcgt tccctcagcc agtcacggtt ctctgcgttc 180
ctggccaaca tttcttcatc cttccagctt gggaggatgg gggagggacc ggtgggagag 240
cccccacctc tccagccccc tgcacttcga cttcatgatt tcctcgtgac actgagaggt 300
agcccagact gggagccaat gctagggctt ctgggagatg tgctggcact cctgggacag 360
gaacagactc cccgggactt tttggtgcac caggcaggtg tactgggtgg acttgtagag 420
gcattgttgg gagcgttagt tcctggaggc ccccctgccc ccactcgacc cccatgcacc 480
cgtgatggcc cttctgactg tgtcctggct gctgattggt tgccttctct gatgttgtta 540
ttagagggta cacgctggca ggccctggtg cagttgcagc ccagtgtgga cccaaccaat 600
gccacaggtc ttgatggtag agagccagct cctcactttt tacagggtct gctgggcttg 660
cttaccccag caggagagtt gggctctgag gaggctcttt ggggtggtct gctgcgcaca 720
gtgggggccc ccctctatgc tgccttccag gaggggctac tgcgagtcac tcattctctg 780
caagatgagg tcttttctat tatgggacag ccagagcctg atgccagtgg gcagtgccag 840
ggaggcaacc ttcaacagct gcttttatgg ggcatgcgga acaacctttc ttgggacgcc 900
cgagcactgg gttttctatc tggatcacca cctccacccc ctgctctcct gcactgcctg 960
agcagaggtg tgcctctgcc cagggcttcc cagcctgcgg ctcacatcag ccctcgacag 1020
cggcgagcca tctctgtgga ggccctctgc gagaaccact caggcccaga gccaccctac 1080
agcatctcca acttctccat ctacttgctc tgccagcaca tcaagcctgc caccccgcgg 1140
ccccctccta ccaccccacg gcctcctcct accaccccac agccccctcc taccactaca 1200
cagcccattc ctgacactac acagccccct cctgtcaccc caaggcctcc tcctaccacc 1260
ccacaacccc ctcctagcac agctgtcatc tgccagacag ctgtatggta cgcagtctcg 1320
tgggcaccag gtgcccgagg ttggctccaa gcctgccatg atcagtttcc tgatcaattt 1380
ctggatatga tctgcggcaa cctctcattt tcagccctgt ctggccccag tcgtcctttg 1440
gtaaagcagc tctgtgctgg cttgctccca ccccccacta gctgtccacc aggcctgatc 1500
cctgtgcccc tcaccccaga aatattctgg ggctgtttcc tggagaatga gacactgtgg 1560
gctgaacggt tgtgtgtgga ggacagtctg caggctgtgc ccccgaggaa ccaggcttgg 1620
gttcagcatg tgtgtcgggg ccccaccttg gacgccactg attttccacc gtgccgcgtt 1680
ggaccctgtg gggaacgctg cccagatggg ggcagcttcc tgctcatggt ctgtgccaat 1740
gacactctgt atgaagcctt ggttcccttc tgggcttggc tagcaggcca atgcagaatt 1800
agtcgtggag gaaatgatac ttgctttcta gaaggcatgc tgggcccctt gttgccctct 1860
ctgccccctc tgggaccatc cccactctgt ctggctcctg gtccttttct gcttggcatg 1920
ttatcccagt tgccacgctg tcagtcctcc gtgccagccc tcgcccaccc cacgcgccta 1980
cattacctcc tgcgcctact gaccttcctt ctgggtccag ggactggggg tgccgagacg 2040
caggggatgt taggtcaagc cctgctgctc tctagtctcc cagacaactg ttcattctgg 2100
gatgccttcc gcccagaggg ccggagaagt gtactgagga cagtcggaga gtacttgcag 2160
cgggaagagc caaccccacc aggcttagac tcctccctca gcctcggctc tggtatgagc 2220
aagatggagc ttctgtcc 2238
<210> 57
<211> 3201
<212> DNA
<213> Homo sapiens
<400> 57
tgctttagtc ctgtgctgtg ggatctgctc cagagggaaa agagtgtttg ggccctgcag 60
attctagtgc aggcgtacct gcatatgccc ccagaaaacc tccagcagct ggtgctttca 120
gcagagaggg aggctgcaca gggcttcctg acactcatgc tgcaggggaa gctgcagggg 180
aagctgcagg taccaccatc cgaggagcag gccctgggtc gcctgacagc cctgctgctc 240
cagcggtacc cacgcctcac ctcccagctc ttcattgacc tgtcaccact catccctttc 300
ttggctgtct ctgacctgat gcgcttccca ccatccctgt tagccaacga cagtgtcctg 360
gctgccatcc gggattacag cccaggaatg aggcctgaac agaaggaggc tctggcaaag 420
cgactgctgg cccctgaact gtttggggaa gtgcctgcct ggccccagga gctgctgtgg 480
gcagtgctgc ccctgctccc ccacctccct ctggagaact ttttgcagct cagccctcac 540
cagatccagg ccctggagga tagctggcca gcagcaggtc tggggccagg gcatgcccgc 600
catgtgctgc gcagcctggt aaaccagagt gtccaggatg gtgaggagca ggtacgcagg 660
cttgggcccc tcgcctgttt cctgagccct gaggagctgc agagcctagt gcccctgagt 720
gatccaacgg ggccagtaga acgggggctg ctggaatgtg cagccaatgg gaccctcagc 780
ccagaaggac gggtggcata tgaacttctg ggtgtgttgc gctcatctgg aggagcggtg 840
ctgagccccc gggagctgcg ggtctgggcc cctctcttct ctcagctggg cctccgcttc 900
cttcaggagc tgtcagagcc ccagcttaga gccatgcttc ctgtcctgca gggaactagt 960
gttacacctg ctcaggctgt cctgctgctt ggacggctcc ttcctaggca cgatctatcc 1020
ctggaggaac tctgctcctt gcaccttctg ctaccaggcc tcagccccca gacactccag 1080
gccatcccta ggcgagtcct ggtcggggct tgttcctgcc tggcccctga actgtcacgc 1140
ctctcagcct gccagaccgc agcactgctg cagacctttc gggttaaaga tggtgttaaa 1200
aatatgggta caacaggtgc tggtccagct gtgtgtatcc ctggtcagcc tattcccacc 1260
acctggccag actgcctgct tcccctgctc ccattaaagc tgctacaact ggattccttg 1320
gctcttctgg caaatcgaag acgctactgg gagctgccct ggtctgagca gcaggcacag 1380
tttctctgga agaagatgca agtacccacc aaccttaccc tcaggaatct gcaggctctg 1440
ggcaccctgg caggaggcat gtcctgtgag tttctgcagc agatcaactc catggtagac 1500
ttccttgaag tggtgcacat gatctatcag ctgcccacta gagttcgagg gagcctgagg 1560
gcctgtatct gggcagagct acagcggagg atggcaatgc cagaaccaga atggacaact 1620
gtagggccag aactgaacgg gctggatagc aagctactcc tggacttacc gatccagttg 1680
atggacagac tatccaatga atccattatg ttggtggtgg agctggtgca aagagctcca 1740
gagcagctgc tggcactgac ccccctccac caggcagccc tggcagagag ggcactacaa 1800
aacctggctc caaaggagac tccagtctca ggggaagtgc tggagacctt aggccctttg 1860
gttggattcc tggggacaga gagcacacga cagatccccc tacagatcct gctgtcccat 1920
ctcagtcagc tgcaaggctt ctgcctagga gagacatttg ccacagagct gggatggctg 1980
ctattgcagg agtctgttct tgggaaacca gagttgtgga gccaggatga agtagagcaa 2040
gctggacgcc tagtattcac tctgtctact gaggcaattt ccttgatccc cagggaggcc 2100
ttgggtccag agaccctgga gcggcttcta gaaaagcagc agagctggga gcagagcaga 2160
gttggacagc tgtgtaggga gccacagctt gctgccaaga aagcagccct ggtagcaggg 2220
gtggtgcgac cagctgctga ggatcttcca gaacctgtgc caaattgtgc agatgtacga 2280
gggacattcc cagcagcctg gtctgcaacc cagattgcag agatggagct ctcagacttt 2340
gaggactgcc tgacattatt tgcaggagac ccaggacttg ggcctgagga actgcgggca 2400
gccatgggca aagcaaaaca gttgtggggt cccccccggg gatttcgtcc tgagcagatc 2460
ctgcagcttg gtaggctctt aataggtcta ggagatcggg aactacagga gctgatccta 2520
gtggactggg gagtgctgag caccctgggg cagatagatg gctggagcac cactcagctc 2580
cgcattgtgg tctccagttt cctacggcag agtggtcggc atgtgagcca cctggacttc 2640
gttcatctga cagcgctggg ttatactctc tgtggactgc ggccagagga gctccagcac 2700
atcagcagtt gggagttcag ccaagcagct ctcttcctcg gcaccctgca tctccagtgc 2760
tctgaggaac aactggaggt tctggcccac ctacttgtac tgcctggtgg gtttggccca 2820
atcagtaact gggggcctga gatcttcact gaaattggca ccatagcagc tgggatccca 2880
gacctggctc tttcagcact gctgcgggga cagatccagg gcgttactcc tcttgccatt 2940
tctgtcatcc ctcctcctaa atttgctgtg gtgtttagtc ccatccaact atctagtctc 3000
accagtgctc aggctgtggc tgtcactcct gagcaaatgg cctttctgag tcctgagcag 3060
cgacgagcag ttgcatgggc ccaacatgag ggaaaggaga gcccagaaca gcaaggtcga 3120
agtacagcct ggggcctcca ggactggtca cgaccttcct ggtccctggt attgactatc 3180
agcttccttg gccacctgct a 3201
<210> 58
<211> 3189
<212> DNA
<213> Mus musculus
<400> 58
tgcttcagtc ctgtactgtg ggatctactc cagagagaga agagcgtttg ggccctgagg 60
accctggtga aggcctacct gcgcatgcct ccagaagacc ttcagcagct tgtgctttca 120
gcagagatgg aggctgcaca gggcttcctg acgctcatgc ttcgttcctg ggctaagctg 180
aaggttcaac catccgagga gcaggccatg ggccgcctga cagccttgct gctccagcgg 240
tacccacgcc tcacctccca actctttatc gacatgtcac cgctcatccc cttcctggct 300
gtccctgacc tcatgcgctt cccaccgtcc cttttggcca acgacagtgt cctggctgcc 360
atcagggatc acagctcagg aatgaagcct gaacagaagg aggccctggc aaaacgactg 420
ctggcccctg agctgtttgg agaagtgcct gattggcccc aggagctgct gtgggcagcc 480
ctgcctctgc ttccccatct gcctctggag agctttctcc agctcagccc tcaccagatc 540
caggccctgg aggatagctg gccagtagca gatcttgggc cgggacacgc ccgacatgtg 600
cttcgtagcc tagtaaacca gagcatggag gatggggagg agcaggtgct caggcttggg 660
tccctcgcct gtttcctgag tcctgaggag ctacagagtc tggtgccctt gagtgatcca 720
atggggcctg tagaacaggg tctgctggaa tgtgcggcca atgggaccct cagcccagaa 780
ggacgggtgg catatgaact tctgggagtg ttgcgttcat ctggaggaac tgtcttaagc 840
ccccgagagc tgagggtctg ggcacctctc tttccccagc tgggcctccg cttcctgcag 900
gagctctcag agacccagct tagagccatg cttcctgccc tacagggagc cagtgtcaca 960
cctgcccagg ctgttctgtt gtttggaagg ctccttccta agcatgatct gtccctggag 1020
gaactctgct ccctgcaccc tctcctgcca ggtctcagcc cccagacact ccaggccatc 1080
cctaagagag ttctggttgg tgcttgttcc tgcctgggcc ctgaactgtc aaggctttca 1140
gcttgccaga ttgcagctct gctgcagacc tttcgggtaa aagatggtgt taaaaatatg 1200
ggtgcagcag gtgccggctc agccgtgtgc attcctgggc agcccaccac ttggccagac 1260
tgcctgcttc ccctgctccc attaaagctg ctacagctgg acgctgcagc tcttctggca 1320
aaccgaagac tctatcggca gctgccttgg tctgagcaac aggcacagtt tctctggaag 1380
aaaatgcaag tgcctaccaa cctgagcctg aggaatctgc aggctctggg caacttggca 1440
ggaggcatga cctgcgagtt tctgcagcag atcagctcaa tggttgactt tcttgatgtg 1500
gtacacatgc tctaccagct gcccactggt gttcgagaga gcctgcgggc ctgtatctgg 1560
acagagctac agcggaggat gacaatgcca gagccagagc tgaccaccct agggccagaa 1620
ctgagtgaac ttgacacaaa gctactcctg gacttgccga tccagctgat ggacagattg 1680
tccaatgatt ccattatgtt ggtggtggag atggtccaag gcgctccaga gcagctgctg 1740
gcactgaccc cactccacca gacagccttg gcagagcgag cacttaaaaa cctggctcca 1800
aaggagaccc caatctccaa agaagtgctg gagacactgg gccccttggt tggattcctg 1860
ggaatagaga gcacgcgacg gatcccttta cccattctac tgtctcatct cagtcagctg 1920
cagggcttct gcctaggaga gacatttgcc acagagctgg gatggctgct gttgcaggag 1980
cctgttcttg gaaaaccaga attgtggagc caggatgaaa tagagcaagc tggacgccta 2040
gtattcactc tgtctgctga ggctatttcc tcgatcccca gggaggcttt gggcccagag 2100
acactggaga ggcttctggg aaagcatcaa agctgggagc agagcagagt gggccatctg 2160
tgtggggagt cacagcttgc ccacaagaaa gcagctctgg tagctgggat tgtgcatcca 2220
gctgctgagg gtctccaaga gcctgtacca aactgtgcag acatacgggg aaccttccca 2280
gcggcctggt ctgcgacaca aatctcagag atggaactct cagactttga agactgcctg 2340
tcactatttg ctggagatcc aggacttggt cctgaggaac tacgggcagc catgggcaag 2400
gccaagcagt tgtggggtcc ccctcgagga ttccgtcctg agcagatctt gcagctgggc 2460
cgtctcctga taggtctagg agaacgggaa ctgcaggagc ttaccttggt ggactggggt 2520
gtgctgagca gcctggggca aatagatggc tggagttcca tgcagctccg agccgtggtc 2580
tccagtttcc taaggcagag tggtcggcat gtgagccacc tggacttcat ttatctgaca 2640
gcactgggtt acacagtctg tggattgcga ccagaggagt tacagcacat cagcagttgg 2700
gagtttagcc aagcagctct cttcctgggt agcttgcatc tcccgtgctc tgaggaacag 2760
ctggaagttc tggcctatct ccttgtgttg cctggtggct ttggcccagt cagtaactgg 2820
gggcctgaga tcttcactga aattggcaca atagcagctg gcatcccaga cctggctctt 2880
tcagcattac tgcggggaca gatccaaggc ctgactcctc ttgccatttc tgtcattcct 2940
gctcccaagt ttgcagtggt cttcaacccc atccagttat ctagtctcac caggggtcag 3000
gccgtagctg ttactcctga acagctggcc tatctgagtc ctgagcagcg gcgagcagtt 3060
gcatgggccc aacacgaagg gaaggagatc ccagagcagc tgggtcgaaa ctcagcctgg 3120
ggtctctacg actggttcca agcctcctgg gccctggcat tgcccgtcag catttttggc 3180
cacctatta 3189
<210> 59
<211> 7
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 59
Thr Leu Ala Val Pro Phe Lys
1 5
<210> 60
<211> 9
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 60
Glu Leu Leu Ser Cys Phe Ser Pro Val
1 5
<210> 61
<211> 9
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 61
Gly Ser Leu Ala Cys Phe Leu Ser Pro
1 5
<210> 62
<211> 9
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 62
Glu Leu Leu Ala Cys Phe Ser Pro Val
1 5
<210> 63
<211> 9
<212> PRT
<213> Artificial Sequence
<220>
<223> Description of Artificial Sequence: Synthetic
peptide
<400> 63
Gly Pro Leu Ala Cys Phe Leu Ser Pro
1 5
Claims (47)
- 세포에서 관심 단백질을 발현시키기 위한 이중-벡터 시스템이며,
a) 5'에서 3' 방향으로:
- 관심 단백질의 아미노 말단 (N-말단) 부분을 코딩하는 부분 코딩 서열의 5'-말단에 있는 신호 서열;
- 관심 단백질의 N-말단 부분을 코딩하는 부분 코딩 서열;
- 부분 코딩 서열에 인접하고 그의 하류인 인테인의 아미노 카르복시 말단 단편 (N-인테인)을 코딩하는 서열
을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터; 및
b) 5'에서 3' 방향으로:
- 관심 단백질의 카르복시 말단 (C-말단) 부분을 코딩하는 부분 코딩 서열의 5'-말단에 있는 신호 서열;
- 신호 서열 및 관심 단백질의 C-말단 부분을 코딩하는 부분 코딩 서열이 플랭킹된 인테인의 카르복시 말단 단편 (C-인테인)을 코딩하는 서열;
- 관심 단백질의 C-말단 부분을 코딩하는 부분 코딩 서열
을 포함하는 제2 뉴클레오티드 서열을 포함하는 제2 벡터
를 포함하는 이중-벡터 시스템. - a) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 관심 단백질의 아미노 말단 (N-말단) 부분을 코딩하는 부분 코딩 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 스플릿 인테인-N을 코딩하는 서열;
- 폴리-아데닐화 (폴리A) 신호 서열;
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터; 및
b) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 스플릿 인테인-C를 코딩하는 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 관심 단백질의 카르복시 말단 (C-말단) 부분을 코딩하는 부분 코딩 서열;
- 폴리-아데닐화 (폴리A) 신호 서열;
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제2 뉴클레오티드 서열을 포함하는 제2 벡터
를 포함하는 이중-벡터 시스템. - 제1항 또는 제2항에 있어서, 세포에서 제1 벡터 및 제2 벡터가 각각
a) N-말단에서 C-말단 방향으로:
- 신호 펩티드 서열, 이에 연결된 관심 단백질 서열의 N-말단 부분, 이의 C-말단 단부에서 융합된 N-인테인 단백질 서열
을 포함하는 제1 단백질 서열; 및
b) N-말단에서 C-말단 방향으로:
- 신호 펩티드 서열, 이에 연결된 C-인테인 단백질 서열, 이에 N-말단 단부가 융합된 관심 단백질 서열의 C-말단 부분
을 포함하는 제2 단백질 서열
을 발현하는 것인 이중-벡터 시스템. - 제1항 내지 제3항 중 어느 한 항에 있어서, 관심 단백질의 N-말단 부분 및 관심 단백질의 C-말단 부분이 전장 관심 단백질을 형성하도록 구성된 것인 이중-벡터 시스템.
- 제3항에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 동일한 것인 이중-벡터 시스템.
- 제3항에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 제1 단백질 서열 및 제2 단백질 서열을 세포의 동일한 세포 구획으로 수송하도록 구성된 것인 이중-벡터 시스템.
- 제3항에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 상이하고, 각각의 신호 펩티드 서열이 각각의 단백질 서열을 세포의 동일한 세포 구획으로 지시하는 것인 이중-벡터 시스템.
- 제1항 내지 제3항 중 어느 한 항에 있어서, 제1 벡터 및 제2 벡터가 각각 바이러스 벡터인 이중-벡터 시스템.
- 제8항에 있어서, 바이러스 벡터가 아데노-연관 바이러스 (AAV) 벡터 또는 렌티바이러스인 이중-벡터 시스템.
- 제1항 내지 제4항 중 어느 한 항에 있어서, 관심 단백질이 STRC 단백질인 이중-벡터 시스템.
- 제1항 내지 제4항 중 어느 한 항에 있어서, 신호 서열이 서열식별번호: 9 또는 서열식별번호: 11에 대해 적어도 80% 동일성의 핵산 서열을 포함하거나 또는 신호 서열이 서열식별번호: 10 또는 서열식별번호: 12에 대해 적어도 80% 동일성의 아미노산 서열을 갖는 신호 펩티드 서열을 코딩하는 것인 이중-벡터 시스템.
- 제1항 내지 제4항 중 어느 한 항에 있어서, 관심 단백질의 N-말단 부분이 서열식별번호: 15 또는 서열식별번호: 16을 코딩하는 핵산 서열에 대해 적어도 70% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 15 또는 서열식별번호: 16에 대해 적어도 70% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제1항 내지 제4항 중 어느 한 항에 있어서, N-인테인 서열이 서열식별번호: 13에 대해 적어도 80% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 14에 대해 적어도 80% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제1항 내지 제4항 중 어느 한 항에 있어서, 관심 단백질의 C-말단 부분이 서열식별번호: 23 또는 서열식별번호: 24를 코딩하는 핵산 서열에 대해 적어도 70% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 23 또는 서열식별번호: 24에 대해 적어도 70% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제1항 내지 제4항 중 어느 한 항에 있어서, C-인테인 서열이 서열식별번호: 21 또는 서열식별번호: 46에 대해 적어도 80% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 22 또는 서열식별번호: 49에 대해 적어도 80% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제1항 내지 제4항 중 어느 한 항에 있어서, 제1 뉴클레오티드 서열이 서열식별번호: 5 또는 서열식별번호: 7에 대해 적어도 70% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 6 또는 서열식별번호: 8에 대해 적어도 70% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제1항 내지 제4항 중 어느 한 항에 있어서, 제2 뉴클레오티드 서열이 서열식별번호: 17 또는 서열식별번호: 19에 대해 적어도 70% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 18 또는 서열식별번호: 20에 대해 적어도 70% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 숙주 세포에서 STRC 유전자의 코딩 서열을 발현시키기 위한 벡터 시스템이며, 여기서 코딩 서열은 서열식별번호: 1, 서열식별번호: 3, 서열식별번호: 5, 서열식별번호: 7, 서열식별번호: 17, 서열식별번호: 19, 서열식별번호: 29, 서열식별번호: 31, 서열식별번호: 33 또는 서열식별번호: 38의 STRC 유전자, 서열식별번호: 30 또는 서열식별번호: 32의 mRNA 서열 또는 그의 단편을 포함하는 적어도 1개의 벡터를 포함하는 것인 벡터 시스템.
- 제18항에 있어서, STRC 유전자가 서열식별번호: 2, 서열식별번호: 4, 서열식별번호: 6, 서열식별번호: 8, 서열식별번호: 15, 서열식별번호: 16, 서열식별번호: 18, 서열식별번호: 20, 서열식별번호: 23, 서열식별번호: 24, 서열식별번호: 25, 서열식별번호: 26, 서열식별번호: 36, 서열식별번호: 39 또는 그의 조합의 STRC 단백질을 코딩하는 것인 벡터 시스템.
- 제18항 또는 제19항에 있어서, 숙주 세포에서 STRC 유전자의 코딩 서열을 발현시키기 위한 이중-벡터 시스템을 포함하며, 여기서 코딩 서열은 5' 말단 단편 및 3' 말단 단편을 포함하고, 이중-벡터 시스템은
a) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, STRC 유전자 코딩 서열의 5' 말단 단편;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 인테인의 아미노 말단 단편 (N-인테인)을 코딩하는 서열;
- 폴리-아데닐화 (폴리A) 신호 서열; 및
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제1 뉴클레오티드 서열을 포함하는 제1 벡터; 및
b) 5'에서 3' 방향으로:
- 5'-역전된 말단 반복부 (5'-ITR) 서열;
- 프로모터 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는 신호 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, 인테인의 카르복시 말단 단편 (C-인테인)을 코딩하는 서열;
- 프로모터에 작동가능하게 연결되고 프로모터의 제어 하에 있는, STRC 유전자 코딩 서열의 3' 말단 단편;
- 폴리-아데닐화 (폴리A) 신호 서열; 및
- 3'-역전된 말단 반복부 (3'-ITR) 서열
을 포함하는 제2 뉴클레오티드 서열을 포함하는 제2 벡터
를 포함하는 것인 벡터 시스템. - 제20항에 있어서, 세포에서 제1 벡터 및 제2 벡터가 각각
a) N-말단에서 C-말단 방향으로:
- 신호 펩티드 서열, 이에 연결된 STRC 단백질 서열의 N-말단 부분, 이의 C-말단 단부에서 융합된 N-인테인 단백질 서열
을 포함하는 제1 단백질 서열; 및
b) N-말단에서 C-말단 방향으로:
- 신호 펩티드 서열, 이에 연결된 C-인테인 단백질 서열, 이에 N-말단 단부가 융합된 STRC 단백질 서열의 C-말단 부분
을 포함하는 제2 단백질 서열
을 발현하는 것인 이중-벡터 시스템. - 제20항 또는 제21항에 있어서, STRC 단백질의 N-말단 부분 및 STRC 단백질의 C-말단 부분이 전장 STRC 단백질을 형성하도록 구성된 것인 이중-벡터 시스템.
- 제21항에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 동일한 것인 이중-벡터 시스템.
- 제21항에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 제1 단백질 서열 및 제2 단백질 서열을 동일한 세포 구획으로 수송하도록 구성된 것인 이중-벡터 시스템.
- 제21항에 있어서, 제1 단백질 서열의 신호 펩티드 서열 및 제2 단백질 서열의 신호 펩티드 서열이 상이하고, 각각의 신호 펩티드 서열이 각각의 단백질 서열을 동일한 세포 구획으로 지시하는 것인 이중-벡터 시스템.
- 제20항 또는 제21항에 있어서, 바이러스 벡터가 아데노-연관 바이러스 (AAV) 벡터인 이중-벡터 시스템.
- 제20항 또는 제21항에 있어서, 신호 서열이 서열식별번호: 9 또는 서열식별번호: 11에 대해 적어도 80% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 10 또는 서열식별번호: 12에 대해 적어도 80% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제20항 또는 제21항에 있어서, STRC 단백질의 N-말단 부분이 서열식별번호: 15 또는 서열식별번호: 16을 코딩하는 핵산 서열에 대해 적어도 70% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 6, 서열식별번호: 8, 서열식별번호: 15 또는 서열식별번호: 16에 대해 적어도 70% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제20항 또는 제21항에 있어서, STRC 단백질의 N-말단 부분이 전장 STRC 단백질의 N-말단 단부 부분의 54% 미만을 포함하는 것인 이중-벡터 시스템.
- 제20항 또는 제21항에 있어서, N-인테인 서열이 서열식별번호: 13에 대해 적어도 80% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 14에 대해 적어도 80% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제20항 또는 제21항에 있어서, STRC 단백질의 C-말단 부분이 서열식별번호: 18, 서열식별번호: 20, 서열식별번호: 23 또는 서열식별번호: 24를 코딩하는 핵산 서열에 대해 적어도 70% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 18, 서열식별번호: 20, 서열식별번호: 23 또는 서열식별번호: 24에 대해 적어도 70% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제20항 또는 제21항에 있어서, STRC 단백질의 C-말단 부분이 전장 STRC 단백질의 C-말단 단부 부분의 46% 이상을 포함하는 것인 이중-벡터 시스템.
- 제20항 또는 제21항에 있어서, C-인테인 서열이 서열식별번호: 21에 대해 적어도 80% 동일한 핵산 서열을 포함하거나 또는 서열식별번호: 22에 대해 적어도 80% 동일한 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제20항 또는 제21항에 있어서, 제1 뉴클레오티드 서열이 서열식별번호: 5 또는 서열식별번호: 7에 대해 적어도 70% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 6, 서열식별번호: 8, 서열식별번호: 15 또는 서열식별번호: 16에 대해 적어도 70% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제20항 또는 제21항에 있어서, 제2 뉴클레오티드 서열이 서열식별번호: 17 또는 서열식별번호: 19에 대해 적어도 70% 동일성의 핵산 서열을 포함하거나 또는 서열식별번호: 18, 서열식별번호: 20, 서열식별번호: 23 또는 서열식별번호: 24에 대해 적어도 70% 동일성의 아미노산 서열을 코딩하는 것인 이중-벡터 시스템.
- 제1항 내지 제35항 중 어느 한 항의 벡터 시스템을 함유하는 세포.
- 제1항 내지 제35항 중 어느 한 항의 벡터 시스템 및 제약상 허용되는 비히클을 포함하는 제약 조성물.
- 상염색체 열성 청력 상실의 치료를 필요로 하는 대상체에게 유효량의 제1항 내지 제35항 중 어느 한 항의 이중-벡터 시스템을 투여하는 것을 포함하는, 대상체에서 상염색체 열성 청력 상실을 치료하는 방법.
- 상염색체 열성 청력 상실의 치료를 필요로 하는 대상체에게 제36항의 세포를 투여하는 것을 포함하는, 대상체에서 상염색체 열성 청력 상실을 치료하는 방법.
- 상염색체 열성 청력 상실의 치료를 필요로 하는 대상체에게 제37항의 제약 조성물을 투여하는 것을 포함하는, 대상체에서 상염색체 열성 청력 상실을 치료하는 방법.
- 제38항 내지 제40항 중 어느 한 항에 있어서, 상염색체 열성 청력 상실이 DFNB16인 방법.
- 대상체의 적어도 1개의 세포를 제37항의 제약 조성물과 접촉시키는 것을 포함하는 방법이며, 여기서 접촉은 제1 뉴클레오티드 서열 및 제2 뉴클레오티드 서열을 포함하는 벡터 시스템을 대상체의 적어도 1개의 세포 내로 전달하고, 여기서 접촉된 적어도 1개의 세포는 펩티드 결합에 의해 연결된 단백질의 N-말단 부분 및 단백질의 C-말단 부분을 발현하여 전장 단백질을 형성하는 것인 방법.
- 청력 상실을 특징으로 하는 병리상태 또는 질환의 치료 및/또는 예방을 필요로 하는 대상체에게 유효량의 제1항 내지 제35항 중 어느 한 항에 따른 벡터 시스템, 제36항에 따른 적어도 1개의 세포 또는 제37항에 따른 제약 조성물을 투여하는 것을 포함하는, 청력 상실을 특징으로 하는 병리상태 또는 질환을 치료 및/또는 예방하는 방법.
- 제42항 또는 제43항에 있어서, 적어도 1개의 세포가 내이 세포인 방법.
- 제42항 또는 제43항에 있어서, 적어도 1개의 세포가 내유모 세포 또는 외유모 세포인 방법.
- 제42항 내지 제45항 중 어느 한 항에 있어서, 적어도 1개의 세포가 생체내 또는 시험관내 세포인 방법.
- 제42항 내지 제46항 중 어느 한 항에 있어서, 대상체에서 청각 기능을 개선 또는 회복시키는 방법.
Applications Claiming Priority (3)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| US202062971555P | 2020-02-07 | 2020-02-07 | |
| US62/971,555 | 2020-02-07 | ||
| PCT/US2021/016720 WO2021158854A2 (en) | 2020-02-07 | 2021-02-05 | Large gene vectors and delivery and uses thereof |
Publications (1)
| Publication Number | Publication Date |
|---|---|
| KR20220139924A true KR20220139924A (ko) | 2022-10-17 |
Family
ID=77200426
Family Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| KR1020227030657A KR20220139924A (ko) | 2020-02-07 | 2021-02-05 | 큰 유전자 벡터 및 그의 전달 및 용도 |
Country Status (8)
| Country | Link |
|---|---|
| US (1) | US20230090778A1 (ko) |
| EP (1) | EP4100518A2 (ko) |
| JP (1) | JP2023512824A (ko) |
| KR (1) | KR20220139924A (ko) |
| AU (1) | AU2021216410A1 (ko) |
| BR (1) | BR112022015601A2 (ko) |
| CA (1) | CA3170709A1 (ko) |
| WO (1) | WO2021158854A2 (ko) |
Families Citing this family (4)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| AU2021225035A1 (en) | 2020-02-21 | 2022-10-13 | Akouos, Inc. | Compositions and methods for treating non-age-associated hearing impairment in a human subject |
| WO2023028497A1 (en) * | 2021-08-24 | 2023-03-02 | The Regents Of The University Of California | Compositions and methods comprising lipid associated transmembrane domains |
| CN116836975A (zh) * | 2022-03-25 | 2023-10-03 | 上海玮美基因科技有限责任公司 | 一种耳蜗和/或前庭细胞特异性启动子及其应用 |
| CN117106824A (zh) * | 2022-05-17 | 2023-11-24 | 复旦大学附属眼耳鼻喉科医院 | 一种治疗听力损伤的双载体系统及其应用 |
Family Cites Families (2)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| EP1339427A4 (en) * | 2000-11-01 | 2004-09-15 | Elusys Therapeutics Inc | PROCESS FOR PRODUCING BISPECIFIC MOLECULES BY TRANSEPISSANCE OF PROTEINS |
| EP3265571B1 (en) * | 2015-03-03 | 2022-04-13 | Fondazione Telethon | Multiple vector system and uses thereof |
-
2021
- 2021-02-05 EP EP21751290.4A patent/EP4100518A2/en active Pending
- 2021-02-05 KR KR1020227030657A patent/KR20220139924A/ko unknown
- 2021-02-05 JP JP2022548118A patent/JP2023512824A/ja active Pending
- 2021-02-05 AU AU2021216410A patent/AU2021216410A1/en active Pending
- 2021-02-05 US US17/798,009 patent/US20230090778A1/en active Pending
- 2021-02-05 BR BR112022015601A patent/BR112022015601A2/pt unknown
- 2021-02-05 WO PCT/US2021/016720 patent/WO2021158854A2/en unknown
- 2021-02-05 CA CA3170709A patent/CA3170709A1/en active Pending
Also Published As
| Publication number | Publication date |
|---|---|
| AU2021216410A1 (en) | 2022-09-01 |
| JP2023512824A (ja) | 2023-03-29 |
| EP4100518A2 (en) | 2022-12-14 |
| US20230090778A1 (en) | 2023-03-23 |
| WO2021158854A2 (en) | 2021-08-12 |
| BR112022015601A2 (pt) | 2022-10-11 |
| WO2021158854A3 (en) | 2021-09-10 |
| CA3170709A1 (en) | 2021-08-12 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| AU2022201319B2 (en) | Viral vectors encoding recombinant fviii variants with increased expression for gene therapy of hemophilia a | |
| KR20220139924A (ko) | 큰 유전자 벡터 및 그의 전달 및 용도 | |
| KR102445667B1 (ko) | 항-인유두종바이러스 16 e7 t 세포 수용체 | |
| CN110050063B (zh) | 酸性α-葡萄糖苷酶变体及其用途 | |
| JP2024012440A (ja) | 蝸牛および前庭細胞に核酸を送達するための組成物および方法 | |
| CN111629786A (zh) | 用于编辑rna的组合物和方法 | |
| KR20200010443A (ko) | B형 혈우병 유전자 요법을 위한 증가된 발현을 가지는 재조합 fix 변이체를 암호화하는 바이러스 벡터 | |
| KR102404550B1 (ko) | A형 혈우병의 유전자 요법을 위한 증가된 발현을 갖는 재조합 fviii 변이체를 인코딩하는 바이러스 벡터 | |
| KR20200095462A (ko) | Hbb 유전자 기능 회복을 위한 아데노-연관 바이러스 조성물 및 이의 사용 방법 | |
| CN108913718A (zh) | 一种靶向EGFR vⅢ的CAR-T细胞的制备方法及应用 | |
| CN113544257A (zh) | 中国仓鼠卵巢细胞中内源性逆转录病毒的表征及灭活 | |
| AU2022200678A1 (en) | Nucleic acid molecules containing spacers and methods of use thereof | |
| CN111902164A (zh) | 用于恢复pah基因功能的腺相关病毒组合物及其使用方法 | |
| US20210386870A1 (en) | Fibroblast growth factor 21 (FGF21) gene therapy | |
| CN112449640A (zh) | 使用编码具有增加的表达的重组fviii变体的病毒载体的a型血友病的基因疗法 | |
| CN115916985A (zh) | 用于中枢神经系统障碍的成纤维细胞生长因子21(fgf21)基因疗法 | |
| US20220226501A1 (en) | Insulin gene therapy | |
| WO2020187272A1 (zh) | 一种用于基因治疗的融合蛋白及其应用 | |
| RU2773956C2 (ru) | Вирусные векторы, кодирующие рекомбинантные варианты fix с повышенной экспрессией, для генотерапии гемофилии в | |
| RU2780410C2 (ru) | Варианты кислой альфа-глюкозидазы и их использование | |
| CN114981299A (zh) | 使用编码具有增加的表达的重组fviii变体的病毒载体的a型血友病的基因疗法 | |
| CN117858895A (zh) | 使用表达增强的编码重组fviii变体的病毒载体的血友病a基因疗法 |