JP2023553190A - Pseudomonas strains and their metabolites that control plant diseases - Google Patents
Pseudomonas strains and their metabolites that control plant diseases Download PDFInfo
- Publication number
- JP2023553190A JP2023553190A JP2023545726A JP2023545726A JP2023553190A JP 2023553190 A JP2023553190 A JP 2023553190A JP 2023545726 A JP2023545726 A JP 2023545726A JP 2023545726 A JP2023545726 A JP 2023545726A JP 2023553190 A JP2023553190 A JP 2023553190A
- Authority
- JP
- Japan
- Prior art keywords
- pseudomonas
- bacterial
- rejuagro
- pathotype
- xanthomonas
- Prior art date
- Legal status (The legal status is an assumption and is not a legal conclusion. Google has not performed a legal analysis and makes no representation as to the accuracy of the status listed.)
- Pending
Links
- 239000002207 metabolite Substances 0.000 title claims abstract description 37
- 241000589516 Pseudomonas Species 0.000 title claims description 83
- 208000037265 diseases, disorders, signs and symptoms Diseases 0.000 title claims description 57
- 201000010099 disease Diseases 0.000 title claims description 47
- 238000000034 method Methods 0.000 claims abstract description 107
- 230000001580 bacterial effect Effects 0.000 claims abstract description 84
- 150000001875 compounds Chemical class 0.000 claims abstract description 45
- 230000012010 growth Effects 0.000 claims abstract description 26
- XEKOWRVHYACXOJ-UHFFFAOYSA-N Ethyl acetate Chemical compound CCOC(C)=O XEKOWRVHYACXOJ-UHFFFAOYSA-N 0.000 claims description 87
- VLKZOEOYAKHREP-UHFFFAOYSA-N n-Hexane Chemical compound CCCCCC VLKZOEOYAKHREP-UHFFFAOYSA-N 0.000 claims description 60
- 239000000203 mixture Substances 0.000 claims description 57
- UCSJYZPVAKXKNQ-HZYVHMACSA-N streptomycin Chemical compound CN[C@H]1[C@H](O)[C@@H](O)[C@H](CO)O[C@H]1O[C@@H]1[C@](C=O)(O)[C@H](C)O[C@H]1O[C@@H]1[C@@H](NC(N)=N)[C@H](O)[C@@H](NC(N)=N)[C@H](O)[C@H]1O UCSJYZPVAKXKNQ-HZYVHMACSA-N 0.000 claims description 50
- 241000894006 Bacteria Species 0.000 claims description 46
- 238000000855 fermentation Methods 0.000 claims description 36
- 230000004151 fermentation Effects 0.000 claims description 36
- 239000006228 supernatant Substances 0.000 claims description 35
- 244000070406 Malus silvestris Species 0.000 claims description 29
- 238000004519 manufacturing process Methods 0.000 claims description 29
- 235000007688 Lycopersicon esculentum Nutrition 0.000 claims description 26
- 240000003768 Solanum lycopersicum Species 0.000 claims description 26
- 201000009030 Carcinoma Diseases 0.000 claims description 25
- 229960005322 streptomycin Drugs 0.000 claims description 25
- 235000013399 edible fruits Nutrition 0.000 claims description 23
- 244000000010 microbial pathogen Species 0.000 claims description 23
- 241000196324 Embryophyta Species 0.000 claims description 22
- 241000588694 Erwinia amylovora Species 0.000 claims description 20
- 244000061456 Solanum tuberosum Species 0.000 claims description 19
- 235000002595 Solanum tuberosum Nutrition 0.000 claims description 19
- 241001312420 Pseudomonas mosselii Species 0.000 claims description 18
- 235000020971 citrus fruits Nutrition 0.000 claims description 17
- 239000007788 liquid Substances 0.000 claims description 15
- XLYOFNOQVPJJNP-UHFFFAOYSA-N water Substances O XLYOFNOQVPJJNP-UHFFFAOYSA-N 0.000 claims description 15
- 241000589636 Xanthomonas campestris Species 0.000 claims description 14
- 241000220324 Pyrus Species 0.000 claims description 13
- 241000589652 Xanthomonas oryzae Species 0.000 claims description 12
- 241000207199 Citrus Species 0.000 claims description 11
- 235000009854 Cucurbita moschata Nutrition 0.000 claims description 11
- 240000007817 Olea europaea Species 0.000 claims description 11
- 235000014443 Pyrus communis Nutrition 0.000 claims description 11
- 241000589655 Xanthomonas citri Species 0.000 claims description 11
- 230000001717 pathogenic effect Effects 0.000 claims description 11
- 235000012015 potatoes Nutrition 0.000 claims description 11
- 239000000047 product Substances 0.000 claims description 11
- 241000123650 Botrytis cinerea Species 0.000 claims description 10
- 235000005087 Malus prunifolia Nutrition 0.000 claims description 10
- 235000006040 Prunus persica var persica Nutrition 0.000 claims description 10
- 241001148183 Pseudomonas savastanoi Species 0.000 claims description 10
- 241000589771 Ralstonia solanacearum Species 0.000 claims description 10
- 239000004575 stone Substances 0.000 claims description 10
- 235000020234 walnut Nutrition 0.000 claims description 10
- 241000228452 Venturia inaequalis Species 0.000 claims description 9
- 241000567083 Xanthomonas arboricola Species 0.000 claims description 9
- 235000021016 apples Nutrition 0.000 claims description 9
- 238000009472 formulation Methods 0.000 claims description 9
- 235000021017 pears Nutrition 0.000 claims description 9
- 235000002566 Capsicum Nutrition 0.000 claims description 8
- 241000207836 Olea <angiosperm> Species 0.000 claims description 8
- 241000531155 Pectobacterium Species 0.000 claims description 8
- 241001136168 Clavibacter michiganensis Species 0.000 claims description 7
- 241000219104 Cucurbitaceae Species 0.000 claims description 7
- 241000233622 Phytophthora infestans Species 0.000 claims description 7
- 239000002671 adjuvant Substances 0.000 claims description 7
- 235000008534 Capsicum annuum var annuum Nutrition 0.000 claims description 6
- 240000008384 Capsicum annuum var. annuum Species 0.000 claims description 6
- 240000001980 Cucurbita pepo Species 0.000 claims description 6
- 235000009852 Cucurbita pepo Nutrition 0.000 claims description 6
- 241000589565 Flavobacterium Species 0.000 claims description 6
- 240000007049 Juglans regia Species 0.000 claims description 6
- 235000009496 Juglans regia Nutrition 0.000 claims description 6
- 240000005561 Musa balbisiana Species 0.000 claims description 6
- 241001148142 Pectobacterium atrosepticum Species 0.000 claims description 6
- 241000695353 Pseudomonas soli Species 0.000 claims description 6
- 244000061458 Solanum melongena Species 0.000 claims description 6
- 235000002597 Solanum melongena Nutrition 0.000 claims description 6
- 235000021015 bananas Nutrition 0.000 claims description 6
- 230000000704 physical effect Effects 0.000 claims description 6
- 230000001681 protective effect Effects 0.000 claims description 6
- 235000020354 squash Nutrition 0.000 claims description 6
- 239000004094 surface-active agent Substances 0.000 claims description 6
- 235000013311 vegetables Nutrition 0.000 claims description 6
- 244000291564 Allium cepa Species 0.000 claims description 5
- 235000002732 Allium cepa var. cepa Nutrition 0.000 claims description 5
- 244000144730 Amygdalus persica Species 0.000 claims description 5
- 235000000832 Ayote Nutrition 0.000 claims description 5
- 241000219122 Cucurbita Species 0.000 claims description 5
- 235000009804 Cucurbita pepo subsp pepo Nutrition 0.000 claims description 5
- 235000002767 Daucus carota Nutrition 0.000 claims description 5
- 244000000626 Daucus carota Species 0.000 claims description 5
- 240000007594 Oryza sativa Species 0.000 claims description 5
- 235000007164 Oryza sativa Nutrition 0.000 claims description 5
- 240000005809 Prunus persica Species 0.000 claims description 5
- 244000070968 Saintpaulia ionantha Species 0.000 claims description 5
- 241000520892 Xanthomonas axonopodis Species 0.000 claims description 5
- 235000015136 pumpkin Nutrition 0.000 claims description 5
- 235000009566 rice Nutrition 0.000 claims description 5
- 241001465180 Botrytis Species 0.000 claims description 4
- 241000758791 Juglandaceae Species 0.000 claims description 4
- 239000006002 Pepper Substances 0.000 claims description 4
- 235000016761 Piper aduncum Nutrition 0.000 claims description 4
- 240000003889 Piper guineense Species 0.000 claims description 4
- 235000017804 Piper guineense Nutrition 0.000 claims description 4
- 235000008184 Piper nigrum Nutrition 0.000 claims description 4
- 241000758706 Piperaceae Species 0.000 claims description 4
- 241000208292 Solanaceae Species 0.000 claims description 4
- 241000589634 Xanthomonas Species 0.000 claims description 4
- 241000815873 Xanthomonas euvesicatoria Species 0.000 claims description 4
- 238000003810 ethyl acetate extraction Methods 0.000 claims description 4
- 239000000843 powder Substances 0.000 claims description 4
- 239000004546 suspension concentrate Substances 0.000 claims description 4
- 239000004562 water dispersible granule Substances 0.000 claims description 4
- 241001464977 Clavibacter michiganensis subsp. michiganensis Species 0.000 claims description 3
- 241001646719 Escherichia coli O157:H7 Species 0.000 claims description 3
- 241000589626 Pseudomonas syringae pv. tomato Species 0.000 claims description 3
- QVGXLLKOCUKJST-UHFFFAOYSA-N atomic oxygen Chemical compound [O] QVGXLLKOCUKJST-UHFFFAOYSA-N 0.000 claims description 3
- 229910052760 oxygen Inorganic materials 0.000 claims description 3
- 239000001301 oxygen Substances 0.000 claims description 3
- 241001187100 Dickeya dadantii Species 0.000 claims description 2
- 241000571844 Pectobacterium parmentieri Species 0.000 claims description 2
- 241000087479 Pseudocercospora fijiensis Species 0.000 claims description 2
- 241000521936 Pseudomonas amygdali pv. lachrymans Species 0.000 claims description 2
- 241000317942 Venturia <ichneumonid wasp> Species 0.000 claims description 2
- 241000907138 Xanthomonas oryzae pv. oryzae Species 0.000 claims description 2
- 241000626572 Xanthomonas oryzae pv. oryzicola Species 0.000 claims description 2
- 239000004480 active ingredient Substances 0.000 claims description 2
- 244000000007 bacterial human pathogen Species 0.000 claims description 2
- 208000010824 fish disease Diseases 0.000 claims description 2
- 239000008187 granular material Substances 0.000 claims description 2
- 239000000463 material Substances 0.000 claims description 2
- 241000588702 Pectobacterium carotovorum subsp. carotovorum Species 0.000 claims 7
- 241000589623 Pseudomonas syringae pv. syringae Species 0.000 claims 7
- 241000219998 Philenoptera violacea Species 0.000 claims 3
- 239000000080 wetting agent Substances 0.000 claims 2
- 244000205754 Colocasia esculenta Species 0.000 claims 1
- 235000006481 Colocasia esculenta Nutrition 0.000 claims 1
- 241000233614 Phytophthora Species 0.000 claims 1
- 229920003171 Poly (ethylene oxide) Polymers 0.000 claims 1
- 241001395385 Pseudomonas savastanoi pv. savastanoi Species 0.000 claims 1
- 241000232299 Ralstonia Species 0.000 claims 1
- 125000000217 alkyl group Chemical group 0.000 claims 1
- 239000003674 animal food additive Substances 0.000 claims 1
- 230000015572 biosynthetic process Effects 0.000 claims 1
- 239000003795 chemical substances by application Substances 0.000 claims 1
- 239000002798 polar solvent Substances 0.000 claims 1
- 229920001451 polypropylene glycol Polymers 0.000 claims 1
- 244000005700 microbiome Species 0.000 abstract description 6
- 230000000845 anti-microbial effect Effects 0.000 abstract description 3
- 230000003389 potentiating effect Effects 0.000 abstract description 3
- 239000002609 medium Substances 0.000 description 63
- OKKJLVBELUTLKV-UHFFFAOYSA-N Methanol Chemical compound OC OKKJLVBELUTLKV-UHFFFAOYSA-N 0.000 description 36
- 239000013078 crystal Substances 0.000 description 32
- 229920001817 Agar Polymers 0.000 description 29
- 239000008272 agar Substances 0.000 description 29
- IAZDPXIOMUYVGZ-UHFFFAOYSA-N Dimethylsulphoxide Chemical compound CS(C)=O IAZDPXIOMUYVGZ-UHFFFAOYSA-N 0.000 description 28
- 239000001965 potato dextrose agar Substances 0.000 description 28
- 238000003556 assay Methods 0.000 description 25
- 235000010633 broth Nutrition 0.000 description 25
- 230000000844 anti-bacterial effect Effects 0.000 description 20
- CSCPPACGZOOCGX-UHFFFAOYSA-N Acetone Chemical compound CC(C)=O CSCPPACGZOOCGX-UHFFFAOYSA-N 0.000 description 18
- 229910052739 hydrogen Inorganic materials 0.000 description 17
- 239000000243 solution Substances 0.000 description 15
- 230000005764 inhibitory process Effects 0.000 description 14
- 230000003993 interaction Effects 0.000 description 14
- 230000000694 effects Effects 0.000 description 13
- 241000894007 species Species 0.000 description 13
- 229940041514 candida albicans extract Drugs 0.000 description 12
- 239000000539 dimer Substances 0.000 description 12
- 239000012138 yeast extract Substances 0.000 description 12
- 238000012360 testing method Methods 0.000 description 11
- 235000011430 Malus pumila Nutrition 0.000 description 10
- 235000015103 Malus silvestris Nutrition 0.000 description 10
- FAPWRFPIFSIZLT-UHFFFAOYSA-M Sodium chloride Chemical compound [Na+].[Cl-] FAPWRFPIFSIZLT-UHFFFAOYSA-M 0.000 description 10
- 125000000623 heterocyclic group Chemical group 0.000 description 10
- 229930014626 natural product Natural products 0.000 description 10
- 241000589615 Pseudomonas syringae Species 0.000 description 9
- 230000000443 biocontrol Effects 0.000 description 9
- 208000015181 infectious disease Diseases 0.000 description 9
- HEDRZPFGACZZDS-UHFFFAOYSA-N Chloroform Chemical compound ClC(Cl)Cl HEDRZPFGACZZDS-UHFFFAOYSA-N 0.000 description 8
- 241000589774 Pseudomonas sp. Species 0.000 description 8
- 240000001987 Pyrus communis Species 0.000 description 8
- 239000000287 crude extract Substances 0.000 description 8
- 239000002024 ethyl acetate extract Substances 0.000 description 8
- 244000052769 pathogen Species 0.000 description 8
- 239000012137 tryptone Substances 0.000 description 8
- 238000004458 analytical method Methods 0.000 description 7
- 230000000975 bioactive effect Effects 0.000 description 7
- 238000004128 high performance liquid chromatography Methods 0.000 description 7
- 238000011081 inoculation Methods 0.000 description 7
- PVTHJAPFENJVNC-MHRBZPPQSA-N kasugamycin Chemical compound N[C@H]1C[C@H](NC(=N)C(O)=O)[C@@H](C)O[C@@H]1O[C@H]1[C@H](O)[C@@H](O)[C@@H](O)[C@H](O)[C@@H]1O PVTHJAPFENJVNC-MHRBZPPQSA-N 0.000 description 7
- 241000588701 Pectobacterium carotovorum Species 0.000 description 6
- 238000003776 cleavage reaction Methods 0.000 description 6
- 239000010949 copper Substances 0.000 description 6
- 238000002360 preparation method Methods 0.000 description 6
- 230000035755 proliferation Effects 0.000 description 6
- 230000007017 scission Effects 0.000 description 6
- 239000000725 suspension Substances 0.000 description 6
- 238000004885 tandem mass spectrometry Methods 0.000 description 6
- 108020004465 16S ribosomal RNA Proteins 0.000 description 5
- 241000108056 Monas Species 0.000 description 5
- 239000003242 anti bacterial agent Substances 0.000 description 5
- 230000000843 anti-fungal effect Effects 0.000 description 5
- 244000052616 bacterial pathogen Species 0.000 description 5
- 230000000853 biopesticidal effect Effects 0.000 description 5
- 125000002915 carbonyl group Chemical group [*:2]C([*:1])=O 0.000 description 5
- 238000004895 liquid chromatography mass spectrometry Methods 0.000 description 5
- 239000002420 orchard Substances 0.000 description 5
- 239000000575 pesticide Substances 0.000 description 5
- 108090000623 proteins and genes Proteins 0.000 description 5
- 239000011780 sodium chloride Substances 0.000 description 5
- 239000000126 substance Substances 0.000 description 5
- QYEWAEAWMXRMHB-YFTUCIGFSA-N (4r)-5-[[(3s,6r,9s,12r,15s,18r,21r,22r)-3-[(2s)-butan-2-yl]-6,12-bis(hydroxymethyl)-22-methyl-9,15-bis(2-methylpropyl)-2,5,8,11,14,17,20-heptaoxo-18-propan-2-yl-1-oxa-4,7,10,13,16,19-hexazacyclodocos-21-yl]amino]-4-[[(2s)-2-[[(3r)-3-hydroxydecanoyl]amino] Chemical compound CCCCCCC[C@@H](O)CC(=O)N[C@@H](CC(C)C)C(=O)N[C@H](CCC(O)=O)C(=O)N[C@@H]1[C@@H](C)OC(=O)[C@H]([C@@H](C)CC)NC(=O)[C@@H](CO)NC(=O)[C@H](CC(C)C)NC(=O)[C@@H](CO)NC(=O)[C@H](CC(C)C)NC(=O)[C@@H](C(C)C)NC1=O QYEWAEAWMXRMHB-YFTUCIGFSA-N 0.000 description 4
- PIFFQYJYNWXNGE-UHFFFAOYSA-N 2,4-diacetylphloroglucinol Chemical compound CC(=O)C1=C(O)C=C(O)C(C(C)=O)=C1O PIFFQYJYNWXNGE-UHFFFAOYSA-N 0.000 description 4
- 241000193830 Bacillus <bacterium> Species 0.000 description 4
- 241000233866 Fungi Species 0.000 description 4
- 241000589540 Pseudomonas fluorescens Species 0.000 description 4
- VYPSYNLAJGMNEJ-UHFFFAOYSA-N Silicium dioxide Chemical compound O=[Si]=O VYPSYNLAJGMNEJ-UHFFFAOYSA-N 0.000 description 4
- 241000607479 Yersinia pestis Species 0.000 description 4
- 229940088710 antibiotic agent Drugs 0.000 description 4
- 229910052799 carbon Inorganic materials 0.000 description 4
- 238000009792 diffusion process Methods 0.000 description 4
- 238000001704 evaporation Methods 0.000 description 4
- 238000003818 flash chromatography Methods 0.000 description 4
- 238000004896 high resolution mass spectrometry Methods 0.000 description 4
- 238000000338 in vitro Methods 0.000 description 4
- 230000002401 inhibitory effect Effects 0.000 description 4
- 238000011068 loading method Methods 0.000 description 4
- 125000002496 methyl group Chemical group [H]C([H])([H])* 0.000 description 4
- 239000013642 negative control Substances 0.000 description 4
- 230000005855 radiation Effects 0.000 description 4
- 101150102864 rpoD gene Proteins 0.000 description 4
- 239000000741 silica gel Substances 0.000 description 4
- 229910002027 silica gel Inorganic materials 0.000 description 4
- 238000001228 spectrum Methods 0.000 description 4
- 238000011282 treatment Methods 0.000 description 4
- QTBSBXVTEAMEQO-UHFFFAOYSA-N Acetic acid Chemical compound CC(O)=O QTBSBXVTEAMEQO-UHFFFAOYSA-N 0.000 description 3
- WQZGKKKJIJFFOK-GASJEMHNSA-N Glucose Natural products OC[C@H]1OC(O)[C@H](O)[C@@H](O)[C@@H]1O WQZGKKKJIJFFOK-GASJEMHNSA-N 0.000 description 3
- 241001047487 Pectobacterium carotovorum subsp. brasiliense Species 0.000 description 3
- 241000721592 Pilea inaequalis Species 0.000 description 3
- 101100091878 Plasmodium falciparum (isolate 3D7) rpoC2 gene Proteins 0.000 description 3
- 229920001030 Polyethylene Glycol 4000 Polymers 0.000 description 3
- 241001253546 Pseudomonas entomophila Species 0.000 description 3
- 238000004364 calculation method Methods 0.000 description 3
- 150000001721 carbon Chemical group 0.000 description 3
- 238000012512 characterization method Methods 0.000 description 3
- 238000002447 crystallographic data Methods 0.000 description 3
- 238000013480 data collection Methods 0.000 description 3
- 238000002474 experimental method Methods 0.000 description 3
- 239000008103 glucose Substances 0.000 description 3
- 238000002955 isolation Methods 0.000 description 3
- 230000000813 microbial effect Effects 0.000 description 3
- 239000002773 nucleotide Substances 0.000 description 3
- 125000003729 nucleotide group Chemical group 0.000 description 3
- 239000013641 positive control Substances 0.000 description 3
- 101150029016 rpo3 gene Proteins 0.000 description 3
- 239000000523 sample Substances 0.000 description 3
- 101150117326 sigA gene Proteins 0.000 description 3
- 230000003595 spectral effect Effects 0.000 description 3
- 230000035899 viability Effects 0.000 description 3
- WEEMDRWIKYCTQM-UHFFFAOYSA-N 2,6-dimethoxybenzenecarbothioamide Chemical compound COC1=CC=CC(OC)=C1C(N)=S WEEMDRWIKYCTQM-UHFFFAOYSA-N 0.000 description 2
- QYEWAEAWMXRMHB-UHFFFAOYSA-N 8-Angeloyl-8alpha-4,9-Muuroladiene-1,8-diol Natural products CCCCCCCC(O)CC(=O)NC(CC(C)C)C(=O)NC(CCC(O)=O)C(=O)NC1C(C)OC(=O)C(C(C)CC)NC(=O)C(CO)NC(=O)C(CC(C)C)NC(=O)C(CO)NC(=O)C(CC(C)C)NC(=O)C(C(C)C)NC1=O QYEWAEAWMXRMHB-UHFFFAOYSA-N 0.000 description 2
- 241000251468 Actinopterygii Species 0.000 description 2
- OKTJSMMVPCPJKN-UHFFFAOYSA-N Carbon Chemical group [C] OKTJSMMVPCPJKN-UHFFFAOYSA-N 0.000 description 2
- 241000588724 Escherichia coli Species 0.000 description 2
- 108700039887 Essential Genes Proteins 0.000 description 2
- 241000604777 Flavobacterium columnare Species 0.000 description 2
- 208000032759 Hemolytic-Uremic Syndrome Diseases 0.000 description 2
- 239000006142 Luria-Bertani Agar Substances 0.000 description 2
- CSNNHWWHGAXBCP-UHFFFAOYSA-L Magnesium sulfate Chemical compound [Mg+2].[O-][S+2]([O-])([O-])[O-] CSNNHWWHGAXBCP-UHFFFAOYSA-L 0.000 description 2
- 238000007476 Maximum Likelihood Methods 0.000 description 2
- 101100038261 Methanococcus vannielii (strain ATCC 35089 / DSM 1224 / JCM 13029 / OCM 148 / SB) rpo2C gene Proteins 0.000 description 2
- 238000005481 NMR spectroscopy Methods 0.000 description 2
- 231100000674 Phytotoxicity Toxicity 0.000 description 2
- 239000002202 Polyethylene glycol Substances 0.000 description 2
- 239000004372 Polyvinyl alcohol Substances 0.000 description 2
- 241001646398 Pseudomonas chlororaphis Species 0.000 description 2
- 241001470247 Ralstonia solanacearum K60-1 Species 0.000 description 2
- UIIMBOGNXHQVGW-UHFFFAOYSA-M Sodium bicarbonate Chemical compound [Na+].OC([O-])=O UIIMBOGNXHQVGW-UHFFFAOYSA-M 0.000 description 2
- 230000009418 agronomic effect Effects 0.000 description 2
- 125000003368 amide group Chemical group 0.000 description 2
- 238000009635 antibiotic susceptibility testing Methods 0.000 description 2
- 238000012458 antifungal assay Methods 0.000 description 2
- 238000013459 approach Methods 0.000 description 2
- 125000004429 atom Chemical group 0.000 description 2
- 230000003115 biocidal effect Effects 0.000 description 2
- 239000012681 biocontrol agent Substances 0.000 description 2
- 229960000074 biopharmaceutical Drugs 0.000 description 2
- 238000001360 collision-induced dissociation Methods 0.000 description 2
- 239000012468 concentrated sample Substances 0.000 description 2
- ARUVKPQLZAKDPS-UHFFFAOYSA-L copper(II) sulfate Chemical compound [Cu+2].[O-][S+2]([O-])([O-])[O-] ARUVKPQLZAKDPS-UHFFFAOYSA-L 0.000 description 2
- 238000012258 culturing Methods 0.000 description 2
- 239000012153 distilled water Substances 0.000 description 2
- 238000009826 distribution Methods 0.000 description 2
- 238000001035 drying Methods 0.000 description 2
- 230000009977 dual effect Effects 0.000 description 2
- 230000007613 environmental effect Effects 0.000 description 2
- 239000000284 extract Substances 0.000 description 2
- 101150013736 gyrB gene Proteins 0.000 description 2
- 238000000589 high-performance liquid chromatography-mass spectrometry Methods 0.000 description 2
- 239000001257 hydrogen Substances 0.000 description 2
- LELOWRISYMNNSU-UHFFFAOYSA-N hydrogen cyanide Chemical compound N#C LELOWRISYMNNSU-UHFFFAOYSA-N 0.000 description 2
- KMAKOBLIOCQGJP-UHFFFAOYSA-N indole-3-carboxylic acid Chemical compound C1=CC=C2C(C(=O)O)=CNC2=C1 KMAKOBLIOCQGJP-UHFFFAOYSA-N 0.000 description 2
- 238000002347 injection Methods 0.000 description 2
- 239000007924 injection Substances 0.000 description 2
- 238000001294 liquid chromatography-tandem mass spectrometry Methods 0.000 description 2
- 238000011177 media preparation Methods 0.000 description 2
- 229960000988 nystatin Drugs 0.000 description 2
- VQOXZBDYSJBXMA-NQTDYLQESA-N nystatin A1 Chemical compound O[C@H]1[C@@H](N)[C@H](O)[C@@H](C)O[C@H]1O[C@H]1/C=C/C=C/C=C/C=C/CC/C=C/C=C/[C@H](C)[C@@H](O)[C@@H](C)[C@H](C)OC(=O)C[C@H](O)C[C@H](O)C[C@H](O)CC[C@@H](O)[C@H](O)C[C@](O)(C[C@H](O)[C@H]2C(O)=O)O[C@H]2C1 VQOXZBDYSJBXMA-NQTDYLQESA-N 0.000 description 2
- 101150012629 parE gene Proteins 0.000 description 2
- 238000003359 percent control normalization Methods 0.000 description 2
- 230000003032 phytopathogenic effect Effects 0.000 description 2
- 229920001223 polyethylene glycol Polymers 0.000 description 2
- 229920002451 polyvinyl alcohol Polymers 0.000 description 2
- 238000002953 preparative HPLC Methods 0.000 description 2
- 238000000746 purification Methods 0.000 description 2
- QJBZDBLBQWFTPZ-UHFFFAOYSA-N pyrrolnitrin Chemical compound [O-][N+](=O)C1=C(Cl)C=CC=C1C1=CNC=C1Cl QJBZDBLBQWFTPZ-UHFFFAOYSA-N 0.000 description 2
- 101150085857 rpo2 gene Proteins 0.000 description 2
- 101150090202 rpoB gene Proteins 0.000 description 2
- 238000005070 sampling Methods 0.000 description 2
- 239000002689 soil Substances 0.000 description 2
- 239000008223 sterile water Substances 0.000 description 2
- 229960002385 streptomycin sulfate Drugs 0.000 description 2
- 108010067142 viscosin Proteins 0.000 description 2
- VEPOHXYIFQMVHW-XOZOLZJESA-N 2,3-dihydroxybutanedioic acid (2S,3S)-3,4-dimethyl-2-phenylmorpholine Chemical compound OC(C(O)C(O)=O)C(O)=O.C[C@H]1[C@@H](OCCN1C)c1ccccc1 VEPOHXYIFQMVHW-XOZOLZJESA-N 0.000 description 1
- IGRCWJPBLWGNPX-UHFFFAOYSA-N 3-(2-chlorophenyl)-n-(4-chlorophenyl)-n,5-dimethyl-1,2-oxazole-4-carboxamide Chemical group C=1C=C(Cl)C=CC=1N(C)C(=O)C1=C(C)ON=C1C1=CC=CC=C1Cl IGRCWJPBLWGNPX-UHFFFAOYSA-N 0.000 description 1
- 125000004070 6 membered heterocyclic group Chemical group 0.000 description 1
- 244000003034 Arancio amaro Species 0.000 description 1
- 244000063299 Bacillus subtilis Species 0.000 description 1
- 235000014469 Bacillus subtilis Nutrition 0.000 description 1
- 208000035143 Bacterial infection Diseases 0.000 description 1
- 241000219193 Brassicaceae Species 0.000 description 1
- 102100033029 Carbonic anhydrase-related protein 11 Human genes 0.000 description 1
- 240000004045 Cassia javanica Species 0.000 description 1
- 238000007445 Chromatographic isolation Methods 0.000 description 1
- 241000186650 Clavibacter Species 0.000 description 1
- 241001092040 Crataegus Species 0.000 description 1
- 235000014493 Crataegus Nutrition 0.000 description 1
- 235000009917 Crataegus X brevipes Nutrition 0.000 description 1
- 235000013204 Crataegus X haemacarpa Nutrition 0.000 description 1
- 235000009685 Crataegus X maligna Nutrition 0.000 description 1
- 235000009444 Crataegus X rubrocarnea Nutrition 0.000 description 1
- 235000009486 Crataegus bullatus Nutrition 0.000 description 1
- 235000017181 Crataegus chrysocarpa Nutrition 0.000 description 1
- 235000009682 Crataegus limnophila Nutrition 0.000 description 1
- 240000000171 Crataegus monogyna Species 0.000 description 1
- 235000004423 Crataegus monogyna Nutrition 0.000 description 1
- 235000002313 Crataegus paludosa Nutrition 0.000 description 1
- 235000009840 Crataegus x incaedua Nutrition 0.000 description 1
- 206010012735 Diarrhoea Diseases 0.000 description 1
- 241001515913 Dickeya dadantii 3937 Species 0.000 description 1
- 206010014896 Enterocolitis haemorrhagic Diseases 0.000 description 1
- 241000192125 Firmicutes Species 0.000 description 1
- 241000238631 Hexapoda Species 0.000 description 1
- 241000282412 Homo Species 0.000 description 1
- 101000867841 Homo sapiens Carbonic anhydrase-related protein 11 Proteins 0.000 description 1
- 101001075218 Homo sapiens Gastrokine-1 Proteins 0.000 description 1
- 239000007836 KH2PO4 Substances 0.000 description 1
- QIVBCDIJIAJPQS-VIFPVBQESA-N L-tryptophane Chemical compound C1=CC=C2C(C[C@H](N)C(O)=O)=CNC2=C1 QIVBCDIJIAJPQS-VIFPVBQESA-N 0.000 description 1
- 108010028921 Lipopeptides Proteins 0.000 description 1
- 241000218922 Magnoliophyta Species 0.000 description 1
- 241001465754 Metazoa Species 0.000 description 1
- 241001430197 Mollicutes Species 0.000 description 1
- 241000131448 Mycosphaerella Species 0.000 description 1
- -1 NIH Small Molecule Chemical class 0.000 description 1
- 241000379990 Nakataea oryzae Species 0.000 description 1
- 241000244206 Nematoda Species 0.000 description 1
- 206010034133 Pathogen resistance Diseases 0.000 description 1
- 102220623458 Pentraxin-4_H10C_mutation Human genes 0.000 description 1
- PCNDJXKNXGMECE-UHFFFAOYSA-N Phenazine Natural products C1=CC=CC2=NC3=CC=CC=C3N=C21 PCNDJXKNXGMECE-UHFFFAOYSA-N 0.000 description 1
- 240000001857 Phyllostachys elegans Species 0.000 description 1
- 101100410148 Pinus taeda PT30 gene Proteins 0.000 description 1
- 241000960592 Pseudomonas aeruginosa group Species 0.000 description 1
- 241001008519 Pseudomonas fluorescens A506 Species 0.000 description 1
- 241000467496 Pseudomonas protegens Species 0.000 description 1
- 241000589776 Pseudomonas putida Species 0.000 description 1
- 241000960608 Pseudomonas putida group Species 0.000 description 1
- 235000011400 Pyrus pyrifolia Nutrition 0.000 description 1
- 240000004808 Saccharomyces cerevisiae Species 0.000 description 1
- 241001478482 Saccharothrix syringae Species 0.000 description 1
- 241000555745 Sciuridae Species 0.000 description 1
- 102220608658 Secreted phosphoprotein 24_H10A_mutation Human genes 0.000 description 1
- 238000012300 Sequence Analysis Methods 0.000 description 1
- 239000000589 Siderophore Substances 0.000 description 1
- PMZURENOXWZQFD-UHFFFAOYSA-L Sodium Sulfate Chemical compound [Na+].[Na+].[O-]S([O-])(=O)=O PMZURENOXWZQFD-UHFFFAOYSA-L 0.000 description 1
- VMHLLURERBWHNL-UHFFFAOYSA-M Sodium acetate Chemical compound [Na+].CC([O-])=O VMHLLURERBWHNL-UHFFFAOYSA-M 0.000 description 1
- 206010041925 Staphylococcal infections Diseases 0.000 description 1
- 241000187747 Streptomyces Species 0.000 description 1
- 229930006000 Sucrose Natural products 0.000 description 1
- CZMRCDWAGMRECN-UGDNZRGBSA-N Sucrose Chemical compound O[C@H]1[C@H](O)[C@@H](CO)O[C@@]1(CO)O[C@@H]1[C@H](O)[C@@H](O)[C@H](O)[C@@H](CO)O1 CZMRCDWAGMRECN-UGDNZRGBSA-N 0.000 description 1
- QIVBCDIJIAJPQS-UHFFFAOYSA-N Tryptophan Natural products C1=CC=C2C(CC(N)C(O)=O)=CNC2=C1 QIVBCDIJIAJPQS-UHFFFAOYSA-N 0.000 description 1
- 241000726445 Viroids Species 0.000 description 1
- 241000700605 Viruses Species 0.000 description 1
- 102220531684 WD repeat and coiled-coil-containing protein_H12A_mutation Human genes 0.000 description 1
- 102220540093 WD repeat and coiled-coil-containing protein_H12D_mutation Human genes 0.000 description 1
- 244000235262 X Citroncirus webberi Species 0.000 description 1
- 235000011985 X Citroncirus webberi Nutrition 0.000 description 1
- 241000985670 Xanthomonas arboricola pv. pruni Species 0.000 description 1
- 241000567019 Xanthomonas vesicatoria Species 0.000 description 1
- 238000009825 accumulation Methods 0.000 description 1
- 239000013543 active substance Substances 0.000 description 1
- 230000006978 adaptation Effects 0.000 description 1
- 239000000654 additive Substances 0.000 description 1
- 238000005273 aeration Methods 0.000 description 1
- 150000001408 amides Chemical class 0.000 description 1
- 230000003042 antagnostic effect Effects 0.000 description 1
- 238000011482 antibacterial activity assay Methods 0.000 description 1
- 238000002802 antimicrobial activity assay Methods 0.000 description 1
- 125000003118 aryl group Chemical group 0.000 description 1
- 208000022362 bacterial infectious disease Diseases 0.000 description 1
- WDIHJSXYQDMJHN-UHFFFAOYSA-L barium chloride Chemical compound [Cl-].[Cl-].[Ba+2] WDIHJSXYQDMJHN-UHFFFAOYSA-L 0.000 description 1
- 229910001626 barium chloride Inorganic materials 0.000 description 1
- 235000015278 beef Nutrition 0.000 description 1
- 230000032770 biofilm formation Effects 0.000 description 1
- 238000003766 bioinformatics method Methods 0.000 description 1
- 230000004071 biological effect Effects 0.000 description 1
- 238000011957 budget and coverage analysis Methods 0.000 description 1
- LLSDKQJKOVVTOJ-UHFFFAOYSA-L calcium chloride dihydrate Chemical compound O.O.[Cl-].[Cl-].[Ca+2] LLSDKQJKOVVTOJ-UHFFFAOYSA-L 0.000 description 1
- 230000004663 cell proliferation Effects 0.000 description 1
- 238000005119 centrifugation Methods 0.000 description 1
- 230000002925 chemical effect Effects 0.000 description 1
- 238000011097 chromatography purification Methods 0.000 description 1
- 230000001332 colony forming effect Effects 0.000 description 1
- 239000000470 constituent Substances 0.000 description 1
- 229910000365 copper sulfate Inorganic materials 0.000 description 1
- 229910000366 copper(II) sulfate Inorganic materials 0.000 description 1
- 230000001419 dependent effect Effects 0.000 description 1
- 238000010586 diagram Methods 0.000 description 1
- 238000007865 diluting Methods 0.000 description 1
- ZPWVASYFFYYZEW-UHFFFAOYSA-L dipotassium hydrogen phosphate Chemical compound [K+].[K+].OP([O-])([O-])=O ZPWVASYFFYYZEW-UHFFFAOYSA-L 0.000 description 1
- 229910000396 dipotassium phosphate Inorganic materials 0.000 description 1
- 235000019797 dipotassium phosphate Nutrition 0.000 description 1
- 231100000676 disease causative agent Toxicity 0.000 description 1
- 235000021186 dishes Nutrition 0.000 description 1
- 239000003814 drug Substances 0.000 description 1
- 229940079593 drug Drugs 0.000 description 1
- 238000010828 elution Methods 0.000 description 1
- 230000008029 eradication Effects 0.000 description 1
- 235000013305 food Nutrition 0.000 description 1
- 244000078673 foodborn pathogen Species 0.000 description 1
- 238000013467 fragmentation Methods 0.000 description 1
- 238000006062 fragmentation reaction Methods 0.000 description 1
- 230000002538 fungal effect Effects 0.000 description 1
- 244000053095 fungal pathogen Species 0.000 description 1
- 239000011521 glass Substances 0.000 description 1
- 231100001261 hazardous Toxicity 0.000 description 1
- 230000036541 health Effects 0.000 description 1
- 229940088597 hormone Drugs 0.000 description 1
- 239000005556 hormone Substances 0.000 description 1
- 238000010348 incorporation Methods 0.000 description 1
- 239000002054 inoculum Substances 0.000 description 1
- 150000002500 ions Chemical class 0.000 description 1
- SURQXAFEQWPFPV-UHFFFAOYSA-L iron(2+) sulfate heptahydrate Chemical compound O.O.O.O.O.O.O.[Fe+2].[O-]S([O-])(=O)=O SURQXAFEQWPFPV-UHFFFAOYSA-L 0.000 description 1
- 230000000670 limiting effect Effects 0.000 description 1
- 150000002632 lipids Chemical class 0.000 description 1
- 230000007774 longterm Effects 0.000 description 1
- 229910052943 magnesium sulfate Inorganic materials 0.000 description 1
- WRUGWIBCXHJTDG-UHFFFAOYSA-L magnesium sulfate heptahydrate Chemical compound O.O.O.O.O.O.O.[Mg+2].[O-]S([O-])(=O)=O WRUGWIBCXHJTDG-UHFFFAOYSA-L 0.000 description 1
- 235000019341 magnesium sulphate Nutrition 0.000 description 1
- 230000007246 mechanism Effects 0.000 description 1
- 208000015688 methicillin-resistant staphylococcus aureus infectious disease Diseases 0.000 description 1
- 230000002906 microbiologic effect Effects 0.000 description 1
- 238000012986 modification Methods 0.000 description 1
- 230000004048 modification Effects 0.000 description 1
- 229910000402 monopotassium phosphate Inorganic materials 0.000 description 1
- 235000019796 monopotassium phosphate Nutrition 0.000 description 1
- 238000003012 network analysis Methods 0.000 description 1
- 230000001937 non-anti-biotic effect Effects 0.000 description 1
- 235000015097 nutrients Nutrition 0.000 description 1
- 235000016709 nutrition Nutrition 0.000 description 1
- 210000000056 organ Anatomy 0.000 description 1
- 230000003204 osmotic effect Effects 0.000 description 1
- 229960004368 oxytetracycline hydrochloride Drugs 0.000 description 1
- 230000003071 parasitic effect Effects 0.000 description 1
- 230000036961 partial effect Effects 0.000 description 1
- 150000002988 phenazines Chemical class 0.000 description 1
- 150000002989 phenols Chemical class 0.000 description 1
- 238000013081 phylogenetic analysis Methods 0.000 description 1
- 235000017807 phytochemicals Nutrition 0.000 description 1
- 230000008635 plant growth Effects 0.000 description 1
- 239000005648 plant growth regulator Substances 0.000 description 1
- 244000000003 plant pathogen Species 0.000 description 1
- 229930000223 plant secondary metabolite Natural products 0.000 description 1
- GNSKLFRGEWLPPA-UHFFFAOYSA-M potassium dihydrogen phosphate Chemical compound [K+].OP(O)([O-])=O GNSKLFRGEWLPPA-UHFFFAOYSA-M 0.000 description 1
- 230000001737 promoting effect Effects 0.000 description 1
- 239000003223 protective agent Substances 0.000 description 1
- 102000004169 proteins and genes Human genes 0.000 description 1
- 238000013138 pruning Methods 0.000 description 1
- 229960002132 pyrrolnitrin Drugs 0.000 description 1
- 238000011160 research Methods 0.000 description 1
- 238000002390 rotary evaporation Methods 0.000 description 1
- 102220040233 rs79219465 Human genes 0.000 description 1
- 229930000044 secondary metabolite Natural products 0.000 description 1
- 230000028327 secretion Effects 0.000 description 1
- 230000035945 sensitivity Effects 0.000 description 1
- 238000000926 separation method Methods 0.000 description 1
- 239000001632 sodium acetate Substances 0.000 description 1
- 235000017281 sodium acetate Nutrition 0.000 description 1
- 235000017557 sodium bicarbonate Nutrition 0.000 description 1
- 229910000030 sodium bicarbonate Inorganic materials 0.000 description 1
- 159000000000 sodium salts Chemical class 0.000 description 1
- 229910052938 sodium sulfate Inorganic materials 0.000 description 1
- 235000011152 sodium sulphate Nutrition 0.000 description 1
- 238000007711 solidification Methods 0.000 description 1
- 230000008023 solidification Effects 0.000 description 1
- 239000011877 solvent mixture Substances 0.000 description 1
- 239000007921 spray Substances 0.000 description 1
- 238000005507 spraying Methods 0.000 description 1
- 238000003756 stirring Methods 0.000 description 1
- 239000011550 stock solution Substances 0.000 description 1
- 238000002899 structure database search Methods 0.000 description 1
- 239000005720 sucrose Substances 0.000 description 1
- 230000004083 survival effect Effects 0.000 description 1
- 208000024891 symptom Diseases 0.000 description 1
- 230000009885 systemic effect Effects 0.000 description 1
- MWKJTNBSKNUMFN-UHFFFAOYSA-N trifluoromethyltrimethylsilane Chemical compound C[Si](C)(C)C(F)(F)F MWKJTNBSKNUMFN-UHFFFAOYSA-N 0.000 description 1
- 238000001291 vacuum drying Methods 0.000 description 1
- 230000017260 vegetative to reproductive phase transition of meristem Effects 0.000 description 1
- SBKWAHPUHRUGMG-CVPKQJCRSA-N viscosinamide Chemical compound CCCCCCC[C@@H](O)CC(=O)N[C@@H](CC(C)C)C(=O)N[C@H](CCC(N)=O)C(=O)N[C@@H]1[C@H](C)OC(=O)[C@H]([C@@H](C)CC)NC(=O)[C@@H](CO)NC(=O)[C@H](CC(C)C)NC(=O)[C@@H](CO)NC(=O)[C@H](CC(C)C)NC(=O)[C@@H](C(C)C)NC1=O SBKWAHPUHRUGMG-CVPKQJCRSA-N 0.000 description 1
- SBKWAHPUHRUGMG-UHFFFAOYSA-N viscosinamide Natural products CCCCCCCC(O)CC(=O)NC(CC(C)C)C(=O)NC(CCC(N)=O)C(=O)NC1C(C)OC(=O)C(C(C)CC)NC(=O)C(CO)NC(=O)C(CC(C)C)NC(=O)C(CO)NC(=O)C(CC(C)C)NC(=O)C(C(C)C)NC1=O SBKWAHPUHRUGMG-UHFFFAOYSA-N 0.000 description 1
- 108010040624 viscosinamide Proteins 0.000 description 1
- 244000000028 waterborne pathogen Species 0.000 description 1
- 238000002424 x-ray crystallography Methods 0.000 description 1
Images
Classifications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N1/00—Microorganisms, e.g. protozoa; Compositions thereof; Processes of propagating, maintaining or preserving microorganisms or compositions thereof; Processes of preparing or isolating a composition containing a microorganism; Culture media therefor
- C12N1/20—Bacteria; Culture media therefor
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N1/00—Microorganisms, e.g. protozoa; Compositions thereof; Processes of propagating, maintaining or preserving microorganisms or compositions thereof; Processes of preparing or isolating a composition containing a microorganism; Culture media therefor
- C12N1/20—Bacteria; Culture media therefor
- C12N1/205—Bacterial isolates
-
- A—HUMAN NECESSITIES
- A01—AGRICULTURE; FORESTRY; ANIMAL HUSBANDRY; HUNTING; TRAPPING; FISHING
- A01N—PRESERVATION OF BODIES OF HUMANS OR ANIMALS OR PLANTS OR PARTS THEREOF; BIOCIDES, e.g. AS DISINFECTANTS, AS PESTICIDES OR AS HERBICIDES; PEST REPELLANTS OR ATTRACTANTS; PLANT GROWTH REGULATORS
- A01N43/00—Biocides, pest repellants or attractants, or plant growth regulators containing heterocyclic compounds
- A01N43/34—Biocides, pest repellants or attractants, or plant growth regulators containing heterocyclic compounds having rings with one nitrogen atom as the only ring hetero atom
- A01N43/40—Biocides, pest repellants or attractants, or plant growth regulators containing heterocyclic compounds having rings with one nitrogen atom as the only ring hetero atom six-membered rings
-
- A—HUMAN NECESSITIES
- A01—AGRICULTURE; FORESTRY; ANIMAL HUSBANDRY; HUNTING; TRAPPING; FISHING
- A01N—PRESERVATION OF BODIES OF HUMANS OR ANIMALS OR PLANTS OR PARTS THEREOF; BIOCIDES, e.g. AS DISINFECTANTS, AS PESTICIDES OR AS HERBICIDES; PEST REPELLANTS OR ATTRACTANTS; PLANT GROWTH REGULATORS
- A01N63/00—Biocides, pest repellants or attractants, or plant growth regulators containing microorganisms, viruses, microbial fungi, animals or substances produced by, or obtained from, microorganisms, viruses, microbial fungi or animals, e.g. enzymes or fermentates
- A01N63/20—Bacteria; Substances produced thereby or obtained therefrom
- A01N63/27—Pseudomonas
-
- A—HUMAN NECESSITIES
- A01—AGRICULTURE; FORESTRY; ANIMAL HUSBANDRY; HUNTING; TRAPPING; FISHING
- A01P—BIOCIDAL, PEST REPELLANT, PEST ATTRACTANT OR PLANT GROWTH REGULATORY ACTIVITY OF CHEMICAL COMPOUNDS OR PREPARATIONS
- A01P1/00—Disinfectants; Antimicrobial compounds or mixtures thereof
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07D—HETEROCYCLIC COMPOUNDS
- C07D213/00—Heterocyclic compounds containing six-membered rings, not condensed with other rings, with one nitrogen atom as the only ring hetero atom and three or more double bonds between ring members or between ring members and non-ring members
- C07D213/90—Heterocyclic compounds containing six-membered rings, not condensed with other rings, with one nitrogen atom as the only ring hetero atom and three or more double bonds between ring members or between ring members and non-ring members having more than three double bonds between ring members or between ring members and non-ring members
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07D—HETEROCYCLIC COMPOUNDS
- C07D491/00—Heterocyclic compounds containing in the condensed ring system both one or more rings having oxygen atoms as the only ring hetero atoms and one or more rings having nitrogen atoms as the only ring hetero atoms, not provided for by groups C07D451/00 - C07D459/00, C07D463/00, C07D477/00 or C07D489/00
- C07D491/02—Heterocyclic compounds containing in the condensed ring system both one or more rings having oxygen atoms as the only ring hetero atoms and one or more rings having nitrogen atoms as the only ring hetero atoms, not provided for by groups C07D451/00 - C07D459/00, C07D463/00, C07D477/00 or C07D489/00 in which the condensed system contains two hetero rings
- C07D491/04—Ortho-condensed systems
- C07D491/044—Ortho-condensed systems with only one oxygen atom as ring hetero atom in the oxygen-containing ring
- C07D491/048—Ortho-condensed systems with only one oxygen atom as ring hetero atom in the oxygen-containing ring the oxygen-containing ring being five-membered
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12R—INDEXING SCHEME ASSOCIATED WITH SUBCLASSES C12C - C12Q, RELATING TO MICROORGANISMS
- C12R2001/00—Microorganisms ; Processes using microorganisms
- C12R2001/01—Bacteria or Actinomycetales ; using bacteria or Actinomycetales
- C12R2001/38—Pseudomonas
Landscapes
- Chemical & Material Sciences (AREA)
- Life Sciences & Earth Sciences (AREA)
- Organic Chemistry (AREA)
- Engineering & Computer Science (AREA)
- Health & Medical Sciences (AREA)
- Zoology (AREA)
- Wood Science & Technology (AREA)
- General Health & Medical Sciences (AREA)
- Biotechnology (AREA)
- Plant Pathology (AREA)
- Pest Control & Pesticides (AREA)
- Environmental Sciences (AREA)
- Genetics & Genomics (AREA)
- Microbiology (AREA)
- Bioinformatics & Cheminformatics (AREA)
- Virology (AREA)
- Dentistry (AREA)
- Agronomy & Crop Science (AREA)
- General Engineering & Computer Science (AREA)
- Biochemistry (AREA)
- Biomedical Technology (AREA)
- Tropical Medicine & Parasitology (AREA)
- Medicinal Chemistry (AREA)
- Chemical Kinetics & Catalysis (AREA)
- General Chemical & Material Sciences (AREA)
- Agricultural Chemicals And Associated Chemicals (AREA)
- Micro-Organisms Or Cultivation Processes Thereof (AREA)
- Preparation Of Compounds By Using Micro-Organisms (AREA)
- Nitrogen Condensed Heterocyclic Rings (AREA)
- Pyridine Compounds (AREA)
Abstract
本開示は、様々な作物のための様々な微生物種の増殖を抑制することができる、0617-T307、0917-T305、0917-T306、0917-T307、0118-T319、0318-T327及び0418-T328の新規細菌株、その細胞ブロス及びその細菌株から生産された新規代謝物の使用方法に関する。方法は、式(I)、(II)、及び(III)を有する化合物に対応する菌株から生産される新規で強力な抗菌代謝物の使用を含む。TIFF2023553190000063.tif71162The present disclosure discloses that the present disclosure can suppress the growth of various microbial species for various crops. A novel bacterial strain, its cell broth, and methods of using novel metabolites produced from the bacterial strain. The method involves the use of novel and potent antimicrobial metabolites produced from strains corresponding to compounds having formulas (I), (II), and (III). TIFF2023553190000063.tif71162
Description
本発明は、生物農薬の分野である。特に、本発明は、様々な微生物種の増殖を抑制することができる、シュードモナス属種(Pseudomonas spp)、0617-T307、0917-T305、0917-T306、0917-T307、0118-T319、0318-T327及び0418-T328の7つの新規菌株、その細胞ブロス及び細菌株から生産された新規代謝物に関係する。0617-T307、0917-T305、0917-T306、0917-T307、0118-T319、0318-T327、及び0418-T328のシュードモナス属菌株は、American Type Culture Collection(ATCC)に寄託され、それぞれATCC受託番号PTA-126796、PTA-126797、PTA-126798、PTA-126799、PTA-126800、PTA-126801、及びPTA-126802を有する。 The present invention is in the field of biopesticides. In particular, the present invention is capable of inhibiting the growth of various microbial species, including Pseudomonas spp. and 0418-T328, their cell broths and novel metabolites produced from the bacterial strains. Pseudomonas strains 0617-T307, 0917-T305, 0917-T306, 0917-T307, 0118-T319, 0318-T327, and 0418-T328 have been deposited with the American Type Culture Collection (ATCC), Each ATCC accession number PTA -126796, PTA-126797, PTA-126798, PTA-126799, PTA-126800, PTA-126801, and PTA-126802.
病原微生物によって引き起こされる植物病害は、指数関数的に増加し、費用がかかる。植物病原生物は、真菌、細菌、マイコプラズマ、ウイルス、ウイロイド、線虫、又は寄生顕花植物を含む。現在、細菌によって引き起こされる一般的な植物病害は、斑点細菌病、細菌性胴枯病、青枯れ病など14種類ある。火傷病(エルウィニア・アミロボーラ(Erwinia amylovora))、柑橘類がん腫病[キサントモナス・アキソノポディス 病原型シトリ(Xanthomonas axonopodis pv. citri)(Xac)]、細菌性斑点病(BLS)[キサントモナス・キャンペストリス 病原型ベシカトリア(Xanthomonas campestris pv. vesicatoria)(XV-16)]、オリーブがん腫病[シュードモナス・サバスタノイ 病原型サバスタノイ(Pseudomonas savastanoi pv.Savastanoi)(Psv)]、軟腐病(ディケヤー・ダダンティイ(Dickeya dadantii)、ペクトバクテリウム・パルメンティエリ(Pectobacterium parmentieri)、ペクトバクテリウム・アトロセプチカム(Pectobacterium atrosepticum)、ペクトバクテリウム・カロトボラム(Pectobacterium carotovorum)は、破壊的な植物病害である。全米では、火傷病の制御費用は1億ドルを超えると推定されている(Norelliら、(2003))。柑橘類がん腫病については、フロリダ州だけでも、1995年から2005年までの根絶プログラムの実施費用、並びに商業生産者及び壊滅した住宅用柑橘類の住宅所有者への補償で、10億ドルに迫ろうとしている。 Plant diseases caused by pathogenic microorganisms increase exponentially and are costly. Plant pathogenic organisms include fungi, bacteria, mycoplasmas, viruses, viroids, nematodes, or parasitic flowering plants. Currently, there are 14 types of common plant diseases caused by bacteria, including bacterial spot, bacterial blight, and bacterial wilt. fire blight (Erwinia amylovora), citrus carcinoma disease [Xanthomonas axonopodis pv. citri (Xac)], bacterial spot disease (BLS) [Xanthomonas campestris pathogen] vesicatoria (Xanthomonas campestris pv. vesicatoria) (XV-16)], olive carcinoma disease [Pseudomonas savastanoi pv. Dickeya dadantii , Pectobacterium parmentieri, Pectobacterium atrosepticum, Pectobacterium carotovorum, It is a devastating plant disease.In the United States, the cost of controlling fire blight is For citrus carcinoma, the cost of implementing an eradication program from 1995 to 2005 in Florida alone has been estimated to exceed $100 million (Norelli et al. (2003)). And compensation to homeowners whose residential citrus trees have been destroyed is approaching $1 billion.
火傷病は、グラム陰性細菌エルウィニア・アミロボーラの感染によって生じるナシ状果の壊滅的な病害で、欧州、ドイツ、オーストリア、及びスイスなど世界の多くの地域でナシやリンゴに影響を与えている(Chenら、(2009))。火傷病が果樹園全体を枯らすことはほとんどないが、この病害とその制御は、依然として大きな経済的損失をもたらす。太平洋岸北西部及びカリフォルニア州北部では、1991年以降、毎年小規模な発生があり、少なくとも一部の地域では3~4年ごとに大規模な発生を経験している。感染した植物部分を取り除くために剪定すると、樹形が崩れ、将来の生産性が低下するため、軽微な病害の発生であっても費用がかかることがある。例えば、樹齢4年のリンゴ園で台木の胴枯れ病が10%発生した場合、1エーカーあたり最大3,500ドルの損失となる(Norelliら、(2003))。 Fire blight is a devastating disease of pome fruits caused by infection with the gram-negative bacterium Erwinia amylovora that affects pears and apples in many parts of the world, including Europe, Germany, Austria, and Switzerland (Chen (2009)). Although fire blight rarely kills entire orchards, this disease and its control still result in significant economic losses. The Pacific Northwest and northern California have experienced small outbreaks every year since 1991, and at least some areas have experienced large outbreaks every three to four years. Even minor disease outbreaks can be costly, as pruning to remove infected plant parts disrupts tree shape and reduces future productivity. For example, a 10% incidence of rootstock blight in a 4-year-old apple orchard can result in losses of up to $3,500 per acre (Norelli et al. (2003)).
微生物天然物は、農薬として豊富な生物学的化合物を提供してきた(Gwinn、(2018))。しかし、現在の細菌性植物病害の予防法は、効果が限定的である。抗生物質のストレプトマイシン硫酸塩(FireWall, AgroSource, Inc.)及びオキシテトラサイクリン塩酸塩(FireLine, AgroSource, Inc.)は、感染リスクが高い場合にE.アミロボーラ対策として主に使用されてきた製品である。これらの化合物は、ヒト及び動物の健康管理にも使用されているため、これらと同じ抗生物質を作物農業に使用することは、議論の余地がある(Stockwell、(2012))。ストレプトマイシン硫酸塩については、抗生物質耐性に関する懸念から、その使用は制限されている(Vranckenら、(2013))。また、火傷病に対して研究されている抗生物質として、カスガマイシンがある。欠点の一つは、カスガマイシンを頻繁に投与すると、植物が破壊される植物毒性につながることである(Adaskavegら、(2010))。もう一つの欠点は、他の抗生物質と比較して、カスガマイシンの値段が高いことである。そのため、カスガマイシンは他の抗生物質と組み合わせて使用する必要がある。 Microbial natural products have provided a wealth of biological compounds as pesticides (Gwinn, (2018)). However, current methods for preventing bacterial plant diseases have limited effectiveness. The antibiotics streptomycin sulfate (FireWall, AgroSource, Inc.) and oxytetracycline hydrochloride (FireLine, AgroSource, Inc.) are used to treat E. coli when the risk of infection is high. This product has been mainly used as a countermeasure against Amylobora. The use of these same antibiotics in crop agriculture is controversial, as these compounds are also used in human and animal health care (Stockwell, (2012)). Concerns about antibiotic resistance have limited the use of streptomycin sulfate (Vrancken et al. (2013)). Kasugamycin is also an antibiotic being studied for fire blight. One of the disadvantages is that frequent administration of kasugamycin leads to phytotoxicity that destroys plants (Adaskaveg et al. (2010)). Another disadvantage is the high price of kasugamycin compared to other antibiotics. Therefore, kasugamycin must be used in combination with other antibiotics.
ここ数十年、多数の非抗生物質製品が開発され、環境保護庁(EPA)に登録され、全米オーガニックプログラム(NOP)に承認され、火傷病制御のために果樹園経営者に販売されてきた(Tiannaら、(2018))。歴史的に、欧州では、バチルス・サブティリス(Bacillus subtilis)をベースにした2つの製品が火傷病制御に登録されている:QST 713株をベースにしたSerenade(登録商標)及びBD 170菌株をベースにしたBiopro(登録商標)(Brogginiら、(2005))。胞子形成性のバチルス属(Bacillus)をベースとした生物製剤は、その長期間の生存性ゆえに、生物的制御に有利である(Haasら、(2005))。2つのバチルス属をベースとした生物製剤のまずまずの成功は、米国とドイツの多くの野外試験で実証されている(Aldwinckleら、(2002);Kunzら、(2011);Lauxら、(2003))。このことは、E.アミロボーラによる花感染症の制御において、バチルス属種が有望である見込みがあることを示唆する。しかし、バチルス属は感染圧が低い場合にのみ有効である。感染圧が中程度及び高い場合には効果がない。得られた結果は、両生物製品ともに不安定で、病害抑制率は71%から0%の間で変動した(Brogginiら、(2005))。 In recent decades, numerous non-antibiotic products have been developed, registered with the Environmental Protection Agency (EPA), approved by the National Organic Program (NOP), and sold to orchardists for fire blight control. (Tianna et al. (2018)). Historically, two products based on Bacillus subtilis have been registered for fire blight control in Europe: Serenade®, based on the QST 713 strain, and Serenade®, based on the BD 170 strain. Biopro® (Brogini et al. (2005)). Biologics based on sporulating Bacillus are advantageous for biological control due to their long-term viability (Haas et al. (2005)). The reasonable success of two Bacillus-based biologics has been demonstrated in a number of field trials in the United States and Germany (Aldwinckle et al. (2002); Kunz et al. (2011); Laux et al. (2003)). ). This means that E. Our results suggest that Bacillus species hold promise in the control of floral infections caused by Amylobora. However, Bacillus species are only effective when the infection pressure is low. It is not effective when the infection pressure is moderate and high. The results obtained were unstable for both biological products, with disease control rates varying between 71% and 0% (Brogini et al. (2005)).
将来の生物学的保護製品は、一方ではE.アミロボーラと効果的に競合し、他方では標的植物の異なる器官上の同じ微小環境にコロニー形成することができなければならない。保護細菌は、病原菌に影響を与える二次代謝産物を生産し、餌と空間を奪い合い、植物との関係性においてE.アミロボーラによる発病を防ぐ。この問題では、シュードモナス属の細菌は、上記の生物学的保護因子に適合する(Haasら、(2005))。様々な植物のコロニー形成細菌の種構成の分析は、シュードモナス属の蛍光細菌が広く存在していることを示した。 Future biological protection products will, on the one hand, be based on E. It must be able to compete effectively with Amylobora and on the other hand colonize the same microenvironment on different organs of the target plant. Protective bacteria produce secondary metabolites that affect pathogens, compete for food and space, and protect E. Prevents the onset of disease caused by Amylobora. In this matter, bacteria of the genus Pseudomonas are compatible with the biological protection factors mentioned above (Haas et al. (2005)). Analysis of the species composition of colonizing bacteria of various plants showed that fluorescent bacteria of the genus Pseudomonas are widely present.
フランスでは、健康及び罹病の両方のリンゴの木、ナシ、サンザシに生息する集団の主要構成要素がシュードモナス属種であり、その多くがインビトロでE.アミロボーラの増殖を制限する能力を示すことがわかった(Paulinら、(1978))。しかし、効能を有する代謝物に関する情報はほとんど報告されていない。 In France, the main constituents of populations on both healthy and diseased apple trees, pears and hawthorns are Pseudomonas species, many of which have been tested in vitro with E. It was found to exhibit the ability to limit the growth of Amylobora (Paulin et al. (1978)). However, little information on metabolites with efficacy has been reported.
カリフォルニアでは、Thomsonら(1976)が、ナシの花の保護に有効な3種類の蛍光性シュードモナス属を選抜した(Thomsonら、(1976))。1980年代半ば、カリフォルニアのナシの木の葉から単離されたP.フルオレッセンス(P.fluorescens)菌株A506は、E.アミロボーラの増殖を制限する特徴的な活性及び、リンゴとナシを火傷病から保護する能力を示した(Lindowら、(1996))。P.フルオレッセンスを含む製品BlightBan(登録商標)A506が開発され、1996年から市販されている。カリフォルニア州、オレゴン州、ワシントン州で行われた多くの実験は、リンゴやナシの様々な保護プログラムにおけるこの製剤の有用性を実証した(Johnson、(2000))。 In California, Thomson et al. (1976) selected three fluorescent Pseudomonas species that were effective in protecting pear flowers (Thomson et al. (1976)). In the mid-1980s, P. spp. was isolated from the leaves of a California pear tree. P. fluorescens strain A506 is an E. fluorescens strain A506. It has shown characteristic activity in restricting the growth of Amylobora and the ability to protect apples and pears from fire blight (Lindow et al. (1996)). P. A product containing fluorescence, BrightBan® A506, was developed and has been on the market since 1996. Numerous experiments conducted in California, Oregon, and Washington demonstrated the usefulness of this formulation in various protection programs for apples and pears (Johnson, (2000)).
英国では、シュードモナス・フルオレッセンスの2つの単離株がサンザシの花及び新芽の保護に使用された(Wilsonら、(1992))。 In the UK, two isolates of Pseudomonas fluorescens have been used for the protection of hawthorn flowers and shoots (Wilson et al. (1992)).
イタリアとニュージーランドでは、BO 3371及びBO G19の符号を有するシュードモナス属の2つの菌株の適性が調査された(Galassoら、(2002))。温室条件では、それらはリンゴ及びナシの花及び新芽を保護するのに非常に有効である。例えば、BO3371菌株のナシの新芽に対する相対的な保護効果は87%に達する(Galassoら、(2002))。しかし、得られた結果は必ずしも一貫しておらず、これは開花から開花終了までの期間の長さに結び付いた花の感受性が関係している可能性がある。 In Italy and New Zealand, the suitability of two strains of the genus Pseudomonas with the codes BO 3371 and BO G19 was investigated (Galasso et al. (2002)). In greenhouse conditions they are very effective in protecting apple and pear flowers and shoots. For example, the relative protective effect of strain BO3371 on pear shoots reaches 87% (Galasso et al. (2002)). However, the results obtained are not always consistent, and this may be related to flower sensitivity linked to the length of the period from anthesis to the end of anthesis.
ニュージーランドでは、蛍光性シュードモナス属種IPV-BO G19菌株が、野外条件下で79%のリンゴの花を保護した。別の実験果樹園では、「Braeburn」リンゴの花にE.アミロボーラを接種する24時間前に散布した場合、蛍光性シュードモナス属種IPV-BO G19及びIPV-BO 3371は、火傷病の発生をそれぞれ78%と58%抑制した(Biondiら、(2006))。 In New Zealand, the fluorescent Pseudomonas sp. IPV-BO G19 strain protected 79% of apple flowers under field conditions. In another experimental orchard, 'Braeburn' apple blossoms have E. When applied 24 hours before inoculation with Amylobora, fluorescent Pseudomonas sp. IPV-BO G19 and IPV-BO 3371 inhibited fire blight outbreaks by 78% and 58%, respectively (Biondi et al. (2006)).
スペインでは、菌株EPS62e P.フルオレッセンスが、野外アッセイにおいてリンゴの花、ナシの果実及びナシの花に対する試験における火傷病を有意に抑制した。P.フルオレッセンス EPS62eの、火傷病に対する適応力及び効力の向上は、栄養強化及び浸透圧適応を組み合わせた戦略によって得られた。生理学的に改良されたP.フルオレッセンス EPS62eをナシの花に対する野外処理は、90%もの高い効果を生じたが、結果は試験によって異なった(Cabrefigaら、(2011);Mikicinskiら、(2020))。 In Spain, strain EPS62e P. Fluorescence significantly suppressed fire blight in tests on apple flowers, pear fruits, and pear flowers in field assays. P. Increased adaptability and efficacy of F. EPS62e against fire blight was obtained by a combined strategy of nutritional fortification and osmotic adaptation. Physiologically improved P. Field treatments of P. fluorescens EPS62e on pear flowers produced efficacy as high as 90%, but results varied between trials (Cabrefiga et al. (2011); Mikicinski et al. (2020)).
ポーランドでは、リンゴの葉圏と土壌から、ナシ果実への火傷病の影響を軽減することができる細菌の47コロニーが単離された(Mikicinskiら、(2008))。 In Poland, 47 colonies of bacteria were isolated from apple phyllosphere and soil that can reduce the impact of fire blight on pear fruits (Mikicinski et al. (2008)).
グラム陰性シュードモナス属種によって生産される代謝物は、包括的に概説されている(Masscheleinら、(2017))。シュードモナス属代謝物の種類は、フェノール化合物、フェナジン、リポペプチドなどに分類される。シュードモナス属種及びその代謝物の機能としては、以下が挙げられる(Alsohimら、(2014)):1)ホルモンを生産する又は全身抵抗性を誘導する;2)天然に存在する多くの菌株も植物の生育を著しく改善する(植物成長調節物質、IAA、ビスコシン)、3)シデロフォアとビスコシン及びビスコシンアミドなどの界面活性物質との生産、並びにシアン化水素、フェナジン、ピロルニトリン又は2,4-ジアシルホログルシノール(DAPG)などの抗菌化合物により拮抗作用が付与され得る。本発明者らの研究では、菌株が同定され、発酵物及び新規代謝物が細菌から生産されており、特にRejuAgro A及びRejuAgro Bは、これまで報告されていない細菌及び真菌を含む複数の病原微生物に対して高い効力を示す。 Metabolites produced by Gram-negative Pseudomonas species have been comprehensively reviewed (Maschelein et al. (2017)). The types of Pseudomonas metabolites are classified into phenolic compounds, phenazines, lipopeptides, and the like. Functions of Pseudomonas species and their metabolites include (Alsohim et al. (2014)): 1) produce hormones or induce systemic resistance; 2) many naturally occurring strains also (plant growth regulators, IAA, viscosin), 3) production of siderophores and surfactants such as viscosin and viscosinamide, as well as hydrogen cyanide, phenazine, pyrrolnitrine or 2,4-diacylhologlucinol ( Antagonistic effects can be imparted by antimicrobial compounds such as DAPG). In our research, bacterial strains have been identified and fermented products and novel metabolites have been produced from bacteria, and in particular, RejuAgro A and RejuAgro B have been shown to be effective against multiple pathogenic microorganisms, including hitherto unreported bacteria and fungi. Shows high efficacy against.
作物の病気を引き起こす様々な病原菌の増殖を阻害することができる、新規の菌株、細胞ブロス、及びそのような菌株から生産される新規の代謝物に由来する新しい生物農薬が、必要とされている。 There is a need for new biopesticides derived from novel bacterial strains, cell broths, and novel metabolites produced from such strains that can inhibit the growth of various pathogenic bacteria that cause crop diseases. .
(発明の簡単な要旨)
第1の態様において、保護代謝物の生産を促進するために細菌を増殖させる方法が提供される。本方法は、代替ステップを含む。1つの方法において、容器中の液体培地中でシュードモナス属細菌を増殖させて、細菌発酵物を生産するステップを提供する。培地体積と容器体積との比は約1:2~1:10の間であり、容器は約100~250RPMの間の速度で振盪される。代替ステップによれば、本方法は、発酵槽中の液体培地中でシュードモナス属細菌を増殖させて、細菌発酵物を生産することを含む。発酵槽の空気流量は、約1~3L/分の間である。溶存酸素の濃度は、5mg/L~12mg/Lの間である。
(Brief summary of the invention)
In a first aspect, a method of growing bacteria to promote production of protective metabolites is provided. The method includes alternative steps. One method provides the step of growing Pseudomonas bacteria in a liquid medium in a container to produce a bacterial ferment. The ratio of medium volume to container volume is between about 1:2 and 1:10, and the container is shaken at a speed between about 100 and 250 RPM. According to an alternative step, the method includes growing Pseudomonas bacteria in a liquid medium in a fermentor to produce a bacterial ferment. The fermentor air flow rate is between about 1 and 3 L/min. The concentration of dissolved oxygen is between 5 mg/L and 12 mg/L.
第2の態様において、細菌発酵物又は保護上清を含む農業用組成物が提供される。農業用組成物は、第1の態様の方法及び第1の態様に関して開示された点のいずれかに従って生産される。第1の点において、農業用組成物は、アジュバントをさらに含む。この点において、アジュバントは、界面活性物質である。 In a second aspect, an agricultural composition comprising a bacterial fermentation or a protected supernatant is provided. The agricultural composition is produced according to the method of the first aspect and any of the points disclosed in relation to the first aspect. In the first respect, the agricultural composition further comprises an adjuvant. In this respect, adjuvants are surfactants.
第3の態様において、細菌性作物病害を制御する方法が提供される。本方法は、いくつかのステップを含む。第1のステップは、第1の態様又はそのいずれかの点で生産された細菌発酵物又は保護上清を含む農業用組成物を生産することを含む。第2のステップは、病原微生物の増殖を抑制するために、前記農業用組成物を作物に適用することを含む。 In a third aspect, a method of controlling bacterial crop diseases is provided. The method includes several steps. The first step comprises producing an agricultural composition comprising the bacterial fermentation or protected supernatant produced in accordance with the first aspect or any point thereof. The second step involves applying the agricultural composition to the crop to inhibit the growth of pathogenic microorganisms.
第4の態様において、細菌性作物病害を制御する方法が提供される。本方法は、1つのステップを含む。ステップは、病原微生物の増殖を抑制するために、約1.0×105~1.0×109cfu/mLの間のシュードモナス属細菌を含む農業用組成物を作物に適用することを含む。 In a fourth aspect, a method of controlling bacterial crop diseases is provided. The method includes one step. The step includes applying to the crop an agronomic composition comprising between about 1.0×10 5 and 1.0×10 9 cfu/mL of Pseudomonas bacteria to inhibit growth of pathogenic microorganisms. .
第5の態様において、シュードモナス属細菌由来の保護代謝物を精製する方法が提供される。本方法は、いくつかのステップを含む。第1のステップは、第1の態様の方法及びその点によって細菌発酵物又は保護上清を生産することを含む。第2のステップは、類似の極性又は特性を有する溶媒混合物によって細菌発酵物又は保護上清を抽出することを含む。第3のステップは、細菌発酵物又は保護上清をヘキサン及び酢酸エチルの混合物を用いて溶出することによって、又は細菌発酵物又は保護上清をヘキサン及び酢酸エチルの混合物を用いて溶出することによって、保護代謝物を含む溶出液を生産することを含む。 In a fifth aspect, a method is provided for purifying a protected metabolite from a Pseudomonas bacterium. The method includes several steps. The first step comprises producing a bacterial fermentation or protected supernatant according to the method of the first aspect and in that respect. The second step involves extracting the bacterial fermentation or protected supernatant with a solvent mixture of similar polarity or properties. The third step is to elute the bacterial fermentation or protected supernatant with a mixture of hexane and ethyl acetate, or by eluting the bacterial fermentation or protected supernatant with a mixture of hexane and ethyl acetate. , including producing an eluate containing the protected metabolite.
第6の態様において、シュードモナス属細菌由来の保護代謝物を含む農業用組成物は、第5の態様の方法及びその点によって精製される。 In a sixth aspect, an agricultural composition comprising a protected metabolite from a Pseudomonas bacterium is purified by the method of and in respect of the fifth aspect.
第7の態様において、細菌性作物病害を制御する方法が提供される。本方法は、いくつかのステップを含む。第1のステップは、第5の態様の方法又はそのいずれかの点によって精製されたシュードモナス属細菌由来の保護代謝物を含む農業用組成物を生産することを含む。第2のステップは、保護上清又はその代謝物の製剤が、溶液(SL)、可溶性粉末(SP)、可溶性顆粒(SG)及びカプセル化製剤であり得る、前記農業用組成物を適用することを含む。さらに、細菌発酵物及び細胞の製剤の農業用組成物は、懸濁濃縮物(SC)、湿潤性粉末(WP)、及び水分散性顆粒(WG)であり得る。 In a seventh aspect, a method of controlling bacterial crop diseases is provided. The method includes several steps. The first step comprises producing an agricultural composition comprising a protected metabolite derived from a Pseudomonas bacterium purified by the method of the fifth aspect or any point thereof. The second step is applying said agricultural composition, wherein the formulation of the protective supernatant or its metabolites can be a solution (SL), soluble powder (SP), soluble granule (SG) and encapsulated formulation. including. Additionally, agricultural compositions of bacterial ferments and cell preparations can be suspension concentrates (SC), wettable powders (WP), and water-dispersible granules (WG).
第8の態様において、結晶性化合物は、以下の構造の1つから選択される。 In an eighth aspect, the crystalline compound is selected from one of the following structures.
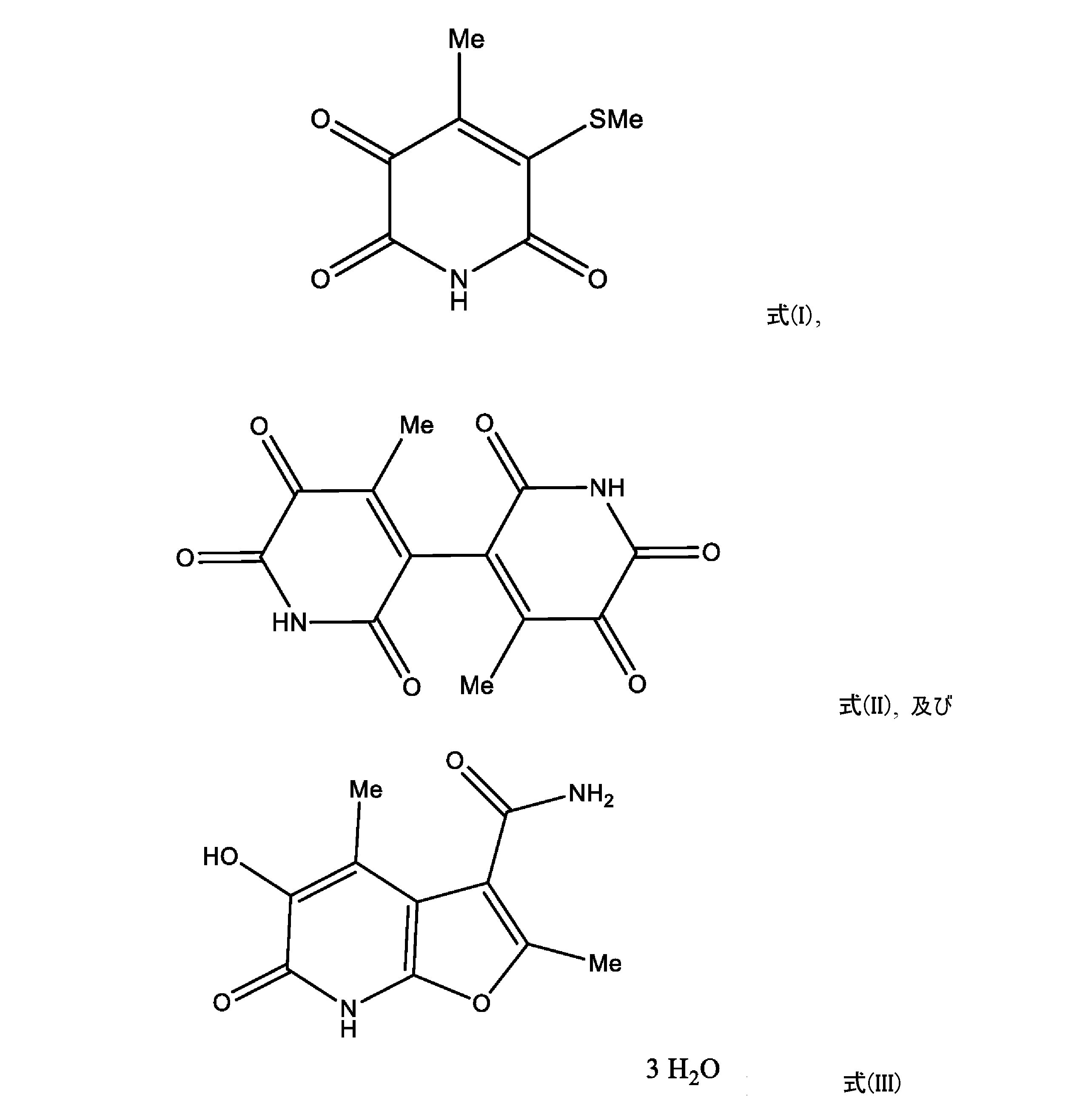
本発明は、本特許に記載されている0617-T307などのシュードモナス属7菌株が生産する、細菌及び真菌を含む病原微生物に対して抗菌活性を示す新規代謝物に関する。16S rRNA及び他のハウスキーピング遺伝子の配列から、この菌株はシュードモナス・プチダ(Pseudomonas putida)群のシュードモナス・ソリ(Pseudomonas soli)0617-T307であると同定された。0617-T307などの7つの細菌株の細胞ブロスは、以下に示されているように、二量体のRejuAgro BとともにRejuAgro Aと名付けられた新規で強力な6員複素環天然物を含む。 The present invention relates to novel metabolites produced by seven Pseudomonas strains, such as 0617-T307 described in this patent, that exhibit antibacterial activity against pathogenic microorganisms, including bacteria and fungi. From the sequences of 16S rRNA and other housekeeping genes, this strain was identified as Pseudomonas soli 0617-T307 of the Pseudomonas putida group. The cell broths of seven bacterial strains, such as 0617-T307, contain a novel and potent 6-membered heterocyclic natural product named RejuAgro A along with dimeric RejuAgro B, as shown below.
これらの化合物、その生産方法、及び植物微生物病原体の阻害のための用途は、本明細書でより詳細に開示される。 These compounds, their production methods and uses for the inhibition of plant microbial pathogens are disclosed in more detail herein.
定義
本開示の態様又は特定の実施形態の要素を導入する場合、冠詞「a」、「an」、「the」、及び「said」は、要素の1つ以上が存在することを意味することが意図される。用語「含む(comprising)」、「含む(including)」及び「有する(having)」は、包括的であることが意図され、列挙された要素以外の追加の要素が存在してもよいことを意味する。用語「又は」は、特に指定がない限り、特定のリストのいずれか1つの要素を意味し、そのリストの要素の任意の組合せも含む。
DEFINITIONS When introducing elements of an aspect of the present disclosure or a particular embodiment, the articles "a,""an,""the," and "said" may mean that one or more of the elements are present. intended. The terms "comprising", "including" and "having" are intended to be inclusive, meaning that additional elements other than those listed may be present. do. The term "or", unless specified otherwise, means any one element of a particular list and also includes any combination of elements of that list.
本明細書で意図されるように、用語「実質的に」、「ほぼ」、及び「約」並びに同様の用語は、本開示の主題が関係する技術分野において一般的でかつ許容される使用と協調して広い意味を有することが意図される。これらの用語は、これらの特徴の範囲を、提供される正にその数値範囲に制限することなく、記載され、及び特許請求された特定の特徴の説明を可能にすることを意図されることが、本開示を検討する当業者によって理解されるべきである。それに応じて、これらの用語は、記載され、及び特許請求された主題の、実質的でない、又は、重要部分でない修正又は変更が、添付の特許請求の範囲に述べる本発明の範囲内にあることが考えられることを指示するものと解釈されるべきである。 As intended herein, the terms "substantially," "approximately," and "about" and similar terms have common and acceptable uses in the art to which the subject matter of this disclosure pertains. They are intended to have a broad meaning in conjunction. These terms are intended to enable description of the specific features described and claimed without limiting the scope of those features to the precise numerical ranges provided. , should be understood by one of ordinary skill in the art upon reviewing this disclosure. Accordingly, these terms are intended to mean that non-substantive or inconsequential modifications or variations of the subject matter described and claimed fall within the scope of the invention as set forth in the appended claims. should be interpreted as indicating that it is considered possible.
「生物学的制御剤(又はBCA)」は、病原体、雑草、昆虫などの有害生物を、安全で、持続可能で、費用対効果に優れた方法で管理する方法である。これらの薬剤は、有害生物種を標的として環境に導入され、環境中の有害生物の個体数や存在量を減少させることを目的としている。 "Biological control agents (or BCAs)" are a safe, sustainable, and cost-effective way to manage pests such as pathogens, weeds, and insects. These drugs are introduced into the environment to target pest species and are intended to reduce the number and abundance of pests in the environment.
「生物学的製剤」とは、宿主にコロニーを作る生きた微生物(細菌、酵母)の製剤である。これらの微生物は、主に着生期の病原体の蓄積を遅らせるために適用される(Tiannaら、(2018))。 A "biological product" is a preparation of live microorganisms (bacteria, yeast) that colonize a host. These microorganisms are mainly applied to slow down the accumulation of pathogens during the epiphytic phase (Tianna et al. (2018)).
「バイオラショナル(Biorational)」とは、微生物に基づく生物農薬に適用される用語である。これらの生物農薬は、多くの場合、微生物株を発酵させることで作られる。これらの製品の多くは、抗菌活性と抗真菌活性の両方を備えている(Tiannaら、(2018))。 "Biorational" is a term applied to biopesticides based on microorganisms. These biopesticides are often made by fermenting microbial strains. Many of these products have both antibacterial and antifungal activity (Tianna et al. (2018)).
「生物農薬」とは、米国環境保護庁(EPA)によって天然素材由来の農薬と定義され、無害な機構によって有害生物を制御する物質を含む生物化学農薬、生物活性天然物(BNP)を通常生産する微生物からなる微生物農薬、遺伝物質を加えたために植物が生み出す活性を持つ植物組み込み型保護剤に分類される(Gwinn K.D.(2018))。 “Biopesticides” are defined by the U.S. Environmental Protection Agency (EPA) as pesticides derived from natural sources and typically produce biochemical pesticides, biologically active natural products (BNPs), including substances that control pests by non-hazardous mechanisms. It is classified as a microbial pesticide made up of microorganisms that have a chemical effect, and a plant-integrated protective agent that has activity produced by plants due to the addition of genetic material (Gwinn K.D. (2018)).
RejuAgro A、RejuAgro B、RejuAgro Cと呼ばれる化合物は、それぞれ以下に例示する式(I)、(II)、(III)を有する化合物に相当する。 The compounds called RejuAgro A, RejuAgro B, and RejuAgro C correspond to compounds having the formulas (I), (II), and (III) illustrated below, respectively.
第1の態様において、保護代謝物の生産を促進するために細菌を増殖させる方法が提供される。本方法は、代替ステップを含む。1つの方法において、容器中の液体培地中でシュードモナス属細菌を増殖させて、細菌発酵物を生産するステップを提供する。培地体積と容器体積の比は約1:2~1:10の間であり、容器は約100~250RPMの間の速度で振盪される。代替ステップによれば、本方法は、発酵槽中の液体培地中でシュードモナス属細菌を増殖させて、細菌発酵物を生産することを含む。発酵槽の空気流量は、約1~3L/分の間である。1つの点においては、本方法は、一定期間後に細菌から液体培地を分離して、保護代謝物を含む保護上清を生産するステップをさらに含む。第2の点において、細菌は、0617-T307、0917-T305、0917-T306、0917-T307、0118-T319、0318-T327、及び0418-T328から選択されるシュードモナス属菌株を含む。第3の点において、増殖温度は約10℃~35℃の間である。第4の点において、液体培地は、細胞の生産用のLB/YME培地である。第5の点において、液体培地は、RejuAgro Aの生産用のYME培地である。第6の点において、培地体積と容器体積の比は、約1:5~1:10の間である。第7の点において、培地体積と容器体積の比は、約1:7~1:9の間である。第8の点において、培地体積と容器体積の比は、約1:8である。第9の点において、容器は約200~250RPMの間の速度で振盪される。第10の点において、容器は約210~230RPMの間の速度で振盪される。第11の点において、発酵槽の空気流量は約1.5~2.5L/分の間であり、溶存酸素の濃度は5mg/L~12mg/Lの間である。第12の点において、増殖温度は約10℃~20℃の間である。第13の点において、増殖温度は約15℃~17℃の間である。第14の点において、細菌は18時間~7日の期間において増殖される。第15の点において、細菌は7日の期間において増殖される。第16の点において、細菌は1日~2日の間の期間において増殖される。 In a first aspect, a method of growing bacteria to promote production of protective metabolites is provided. The method includes alternative steps. One method provides the step of growing Pseudomonas bacteria in a liquid medium in a container to produce a bacterial ferment. The ratio of medium volume to container volume is between about 1:2 and 1:10, and the container is shaken at a speed between about 100 and 250 RPM. According to an alternative step, the method includes growing Pseudomonas bacteria in a liquid medium in a fermentor to produce a bacterial ferment. The fermentor air flow rate is between about 1 and 3 L/min. In one aspect, the method further includes separating the liquid medium from the bacteria after a period of time to produce a protected supernatant containing protected metabolites. In the second respect, the bacterium comprises a Pseudomonas strain selected from 0617-T307, 0917-T305, 0917-T306, 0917-T307, 0118-T319, 0318-T327, and 0418-T328. In the third point, the growth temperature is between about 10°C and 35°C. In the fourth point, the liquid medium is LB/YME medium for production of cells. In the fifth point, the liquid medium is YME medium for the production of RejuAgro A. In a sixth point, the ratio of medium volume to container volume is between about 1:5 and 1:10. In a seventh point, the ratio of medium volume to container volume is between about 1:7 and 1:9. In the eighth point, the ratio of medium volume to container volume is about 1:8. At the ninth point, the container is shaken at a speed of between about 200-250 RPM. At the tenth point, the container is shaken at a speed of between about 210-230 RPM. In the eleventh point, the fermentor air flow rate is between about 1.5-2.5 L/min and the concentration of dissolved oxygen is between 5 mg/L and 12 mg/L. At the twelfth point, the growth temperature is between about 10°C and 20°C. In the thirteenth point, the growth temperature is between about 15°C and 17°C. In the fourteenth point, the bacteria are grown for a period of 18 hours to 7 days. In the fifteenth point, the bacteria are grown for a period of seven days. In the sixteenth point, the bacteria are grown for a period of between one and two days.
第2の態様において、細菌発酵物又は保護上清を含む農業用組成物が提供される。農業用組成物は、第1の態様の方法及び第1の態様に関して開示された点のいずれかに従って生産される。第1の点において、農業用組成物は、アジュバントをさらに含む。この点で、アジュバントは、界面活性物質である。 In a second aspect, an agricultural composition comprising a bacterial fermentation or a protected supernatant is provided. The agricultural composition is produced according to the method of the first aspect and any of the points disclosed in relation to the first aspect. In the first respect, the agricultural composition further comprises an adjuvant. In this respect, adjuvants are surface-active substances.
第3の態様において、細菌性及び真菌作物病害を制御する方法が提供される。本方法は、いくつかのステップを含む。第1のステップは、第1の態様又はそのいずれかの点で生産された細菌発酵物又は保護上清を含む農業用組成物を生産することを含む。第2のステップは、病原微生物の増殖を抑制するために、前記農業用組成物を作物に適用することを含む。 In a third aspect, a method of controlling bacterial and fungal crop diseases is provided. The method includes several steps. The first step comprises producing an agricultural composition comprising the bacterial fermentation or protected supernatant produced in accordance with the first aspect or any point thereof. The second step involves applying the agricultural composition to the crop to inhibit the growth of pathogenic microorganisms.
第1の点において、作物病害は、火傷病、柑橘類がん腫病、オリーブがん腫病、及び軟腐病、トマト及びコショウからなる群から選択される。第2の点において、病原微生物は、ミコスフェレラ・フィジエンシス、ボトリティス・シネレア、エルウィニア・アミロボーラ(Ea)、キサントモナス・アキソノポディス 病原型シトリ(Xanthomonas axonopodis pv. citri)(Xac)、ペクトバクテリウム・パルメンティエリ、ペクトバクテリウム・アトロセプチカム、ペクトバクテリウム・カロトボラム 亜種ブラシリエンシス(Pectobacterium carotovorum subsp. brasiliensis)、ペクトバクテリウム・カロトボラム 亜種カロトボラム(Pectobacterium carotovorum subsp. carotovorum)、ディケヤー・ダダンティイ、シュードモナス・サバスタノイ 病原型サバスタノイ(Psv)、シュードモナス・シリンガエ 病原型トマト(Pseudomonas syringae pv. tomato)、シュードモナス・シリンガエ 病原型シリンガエ(Pseudomonas syringae pv syringae)、シュードモナス・シリンガエ 病原型ラクリマンス(Pseudomonas syringae pv. lachrymans)、キサントモナス・キャンペストリス 病原型プルニ(Xanthomonas campestris pv. pruni)、キサントモナス・キャンペストリス 病原型ベシカトリア(Xanthomonas campestris pv. vesicatoria)、キサントモナス・アルボリコーラ 病原型ジュグランディス(Xanthomonas arboricola pv. juglandis)、ラルストニア・ソラナセアラム(Ralstonia solanacearum)、クラビバクター・ミシガンエンシス 亜種ミシガンエンシス(Clavibacter michiganensis subsp. michiganensis)、フィトフトラ・インフェスタンス(Phytophthora infestans)、ベンチュリア・イナエキュアリス(Venturia inaequalis)、キサントモナス・オリザエ 病原型オリザエ(Xanthomonas oryzae pv. oryzae)、キサントモナス・オリザエ 病原型オリジコーラ(Xanthomonas oryzae pv. oryzicola)及びキサントモナス・シトリ 病原型シトリ(Xanthomonas citri pv. citri.)、からなる群から選択される。第3の点において、作物は、バナナ、リンゴ、ナシ、クラブアップル、柑橘類、ジャガイモ、カボチャ、タマネギ、コメ、アフリカスミレ;ニンジン、ジャガイモ、トマト、ナス、葉菜類、スカッシュ及びウリ類などのアブラナ科(Cruciferae)、ナス科(Solanaceae)、ウリ科(Cucurbitaceae)の植物種、コショウ及びグリーンペッパー、オリーブ;オリーブ、モモ、クルミを含む石果及びナシ状果植物、の1つ以上から選択される。 In the first respect, the crop disease is selected from the group consisting of fire blight, citrus carcinoma, olive carcinoma, and soft rot, tomato and pepper. In the second respect, the pathogenic microorganisms include Mycospherella fisiensis, Botrytis cinerea, Erwinia amylovora (Ea), Xanthomonas axonopodis pv. citri (Xac), Pectobacterium palmentieri , Pectobacterium atrosepticum, Pectobacterium carotovorum subsp. brasiliensis, Pectobacterium carotovorum subsp. brasiliensis, Pectobacterium carotovorum subsp. orum subsp. carotovorum), Dikeya dadantii, Pseudomonas savastanoi pathotypes savastanoi (Psv), Pseudomonas syringae pv. tomato, Pseudomonas syringae pv syringae, Pseudomonas syringae pv. lacrimans (Pseudomonas syringae pv. lachrymans), Xanthomonas campest Squirrel Xanthomonas campestris pv. pruni, Xanthomonas campestris pv. vesicatoria, Xanthomonas arboricola pv. s arboricola pv. juglandis), Ralstonia solanacearum , Clavibacter michiganensis subsp. michiganensis, Phytophthora infestans, Venturia inaeq ualis), Xanthomonas oryzae pv. oryzae), Xanthomonas oryzae pv. oryzicola, and Xanthomonas citri pv. citri. In the third respect, crops include cruciferous plants such as bananas, apples, pears, crabapples, citrus fruits, potatoes, pumpkins, onions, rice, African violets; carrots, potatoes, tomatoes, eggplants, leafy vegetables, squash and cucurbits; Cruciferae, Solanaceae, Cucurbitaceae, peppers and green peppers, olives; stone fruit and pome fruit plants, including olives, peaches, and walnuts.
第4の態様において、細菌性作物病害を制御する方法が提供される。本方法は、1つのステップを含む。ステップは、病原微生物の増殖を抑制するために、約1.0×105~1.0×109cfu/mLの間のシュードモナス属細菌を含む農業用組成物を作物に適用することを含む。 In a fourth aspect, a method of controlling bacterial crop diseases is provided. The method includes one step. The step includes applying to the crop an agronomic composition comprising between about 1.0×10 5 and 1.0×10 9 cfu/mL of Pseudomonas bacteria to inhibit growth of pathogenic microorganisms. .
第1の点において、シュードモナス属細菌は、0617-T307、0917-T305、0917-T306、0917-T307、0118-T319、0318-T327、及び0418-T328から選択されるシュードモナス属菌株である。第2の点において、組成物は、約5.0×107~2.0×108cfu/mLの間のシュードモナス属細菌を含む。第3の点において、作物病害は、ブラックシガトカ、灰色かび病、火傷病、柑橘類がん腫病、軟腐病、オリーブがん腫病、トマト斑葉細菌病、細菌性がん腫病又はイモチ病(石果及びナシ状果)、ウリ科の角斑病、モモの斑点細菌病、トマト斑点細菌病、クルミ胴枯れ病、青枯れ病、トマトがん腫病、ジャガイモ葉枯れ病、リンゴ赤かび病、白葉枯病、及び条斑細菌病、からなる群から選択される。第4の点において、病原微生物は、ミコスフェレラ・フィジエンシス、ボトリティス・シネレア、エルウィニア・アミロボーラ(Ea)、キサントモナス・アキソノポディス 病原型シトリ(Xac)、ペクトバクテリウム・パルメンティエリ、ペクトバクテリウム・アトロセプチカム、ペクトバクテリウム・カロトボラム 亜種ブラシリエンシス、ペクトバクテリウム・カロトボラム 亜種カロトボラム、ディケヤー・ダダンティイ、シュードモナス・サバスタノイ 病原型サバスタノイ(Psv)、シュードモナス・シリンガエ 病原型トマト、シュードモナス・シリンガエ 病原型シリンガエ、シュードモナス・シリンガエ 病原型ラクリマンス、キサントモナス・キャンペストリス 病原型プルニ、キサントモナス・キャンペストリス 病原型ベシカトリア、キサントモナス・アルボリコーラ 病原型ジュグランディス、ラルストニア・ソラナセアラム、クラビバクター・ミシガンエンシス 亜種ミシガンエンシス、フィトフトラ・インフェスタンス、ベンチュリア・イナエキュアリス、キサントモナス・オリザエ 病原型オリザエ、キサントモナス・オリザエ 病原型オリジコーラ及びキサントモナス・シトリ 病原型シトリ、からなる群から選択される。第5の点において、作物は、バナナ、リンゴ、ナシ、クラブアップル、柑橘類、ジャガイモ、カボチャ、タマネギ、コメ、アフリカスミレ;ニンジン、ジャガイモ、トマト、ナス、葉菜類、スカッシュ及びウリ類などのアブラナ科、ナス科、ウリ科の植物種、コショウ及びグリーンペッパー、オリーブ;オリーブ、モモ、クルミを含む石果及びナシ状果植物、の1つ以上から選択される。 In the first respect, the Pseudomonas bacterium is a Pseudomonas strain selected from 0617-T307, 0917-T305, 0917-T306, 0917-T307, 0118-T319, 0318-T327, and 0418-T328. In a second point, the composition comprises between about 5.0×10 7 and 2.0×10 8 cfu/mL of Pseudomonas bacteria. In the third point, the crop disease is black sigatoka, botrytis blight, fire blight, citrus carcinoma disease, soft rot, olive carcinoma disease, tomato leaf spot bacterial disease, bacterial carcinoma disease or potato blight. diseases (stone fruits and pome fruits), horn spot of cucurbits, bacterial spot of peaches, bacterial spot of tomato, walnut blight, bacterial wilt, tomato carcinoma, potato leaf blight, apple red selected from the group consisting of mildew, leaf blight, and bacterial streak disease. In the fourth point, the pathogenic microorganism is Mycospherella fisiensis, Botrytis cinerea, Erwinia amylovora (Ea), Xanthomonas axonopodis citri (Xac), Pectobacterium palmentieri, Pectobacterium atrosepticum, Pectobacterium carotovorum subspecies brasiliensis, Pectobacterium carotovorum subspecies carotovorum, Dikeya dadantii, Pseudomonas savastanoi Pathotype savastanoi (Psv), Pseudomonas syringae Pathotype tomato, Pseudomonas syringae Pathotype syringae, Pseudomonas savastanoi Syringae Pathotype lacrimans, Xanthomonas campestris Pathotype Pruni, Xanthomonas campestris Pathotype Vesicatoria, Xanthomonas arboricola Pathotype Jugrandis, Ralstonia solanacearum, Clavibacter michiganensis Subspecies michiganensis, Phytophthora infestans, selected from the group consisting of Venturia inaequalis, Xanthomonas oryzae, Pathotype oryzae, Xanthomonas oryzae, Pathotype orydicola, and Xanthomonas citri, Pathotype citri. In the fifth point, the crops include bananas, apples, pears, crabapples, citrus fruits, potatoes, pumpkins, onions, rice, African violets; cruciferous crops such as carrots, potatoes, tomatoes, eggplants, leafy vegetables, squash and cucurbits; selected from one or more of plant species of Solanaceae, Cucurbitaceae, pepper and green pepper, olive; stone fruit and pome fruit plants including olive, peach, walnut.
第5の態様において、シュードモナス属細菌由来の保護代謝物を精製する方法が提供される。本方法は、いくつかのステップを含む。第1のステップは、第1の態様の方法及びその点によって細菌発酵物又は保護上清を生産することを含む。第2のステップは、酢酸エチル抽出によって、細菌発酵物又は保護上清を抽出することを含む。第3のステップは、例えば50%ヘキサンと50%酢酸エチルの混合物など、ヘキサンと酢酸エチルの混合物を用いて細菌発酵物又は保護上清を溶出することにより、又は例えば25%ヘキサンと75%酢酸エチルの混合物など、ヘキサンと酢酸エチルの混合物を用いて酢酸エチル抽出物を溶出することにより、保護代謝物を含む溶出物を生産することを含む。 In a fifth aspect, a method is provided for purifying a protected metabolite from a Pseudomonas bacterium. The method includes several steps. The first step comprises producing a bacterial fermentation or protected supernatant according to the method of the first aspect and in that respect. The second step involves extracting the bacterial fermentation or protected supernatant by ethyl acetate extraction. The third step is by eluting the bacterial fermentation or protected supernatant with a mixture of hexane and ethyl acetate, such as a mixture of 50% hexane and 50% ethyl acetate, or by elution of the bacterial fermentation or protected supernatant, such as a mixture of 25% hexane and 75% acetic acid. eluting the ethyl acetate extract with a mixture of hexane and ethyl acetate, such as a mixture of ethyl acetate, to produce an eluate containing the protected metabolite.
第1の点において、シュードモナス属細菌は、0617-T307、0917-T305、0917-T306、0917-T307、0118-T319、0318-T327、及び0418-T328から選択されるシュードモナス属菌株である。 In the first respect, the Pseudomonas bacterium is a Pseudomonas strain selected from 0617-T307, 0917-T305, 0917-T306, 0917-T307, 0118-T319, 0318-T327, and 0418-T328.
第6の態様において、シュードモナス属細菌由来の保護代謝物を含む農業用組成物は、第5の態様の方法及びその点によって精製される。 In a sixth aspect, an agricultural composition comprising a protected metabolite from a Pseudomonas bacterium is purified by the method of and in respect of the fifth aspect.
第7の態様において、細菌性作物病害を制御する方法が提供される。本方法は、いくつかのステップを含む。第1のステップは、第5の態様の方法又はそのいずれかの点によって精製されたシュードモナス属細菌由来の保護代謝物を含む農業用組成物を生産することを含む。第2のステップは、病原微生物の増殖を抑制するために、前記農業用組成物を作物に適用することを含む。 In a seventh aspect, a method of controlling bacterial crop diseases is provided. The method includes several steps. The first step comprises producing an agricultural composition comprising a protected metabolite derived from a Pseudomonas bacterium purified by the method of the fifth aspect or any point thereof. The second step involves applying the agricultural composition to the crop to inhibit the growth of pathogenic microorganisms.
第1の点において、作物病害は、火傷病、柑橘類がん腫病、オリーブがん腫病、軟腐病、トマト及びコショウからなる群から選択される。第2の点において、病原微生物は、ミコスフェレラ・フィジエンシス、ボトリティス・シネレア、エルウィニア・アミロボーラ(Ea)(特にストレプトマイシン耐性E.アミロボーラ菌株)、キサントモナス・アキソノポディス 病原型シトリ(Xac)、ペクトバクテリウム・パルメンティエリ、ペクトバクテリウム・アトロセプチカム、ペクトバクテリウム・カロトボラム 亜種ブラシリエンシス、ペクトバクテリウム・カロトボラム 亜種カロトボラム、ディケヤー・ダダンティイ、シュードモナス・サバスタノイ 病原型サバスタノイ(Psv)、シュードモナス・シリンガエ 病原型トマト、シュードモナス・シリンガエ 病原型シリンガエ、シュードモナス・シリンガエ 病原型ラクリマンス、キサントモナス・キャンペストリス 病原型プルニ、キサントモナス・キャンペストリス 病原型ベシカトリア、キサントモナス・アルボリコーラ 病原型ジュグランディス、ラルストニア・ソラナセアラム、クラビバクター・ミシガンエンシス 亜種ミシガンエンシス、フィトフトラ・インフェスタンス、ベンチュリア・イナエキュアリス、キサントモナス・オリザエ 病原型オリザエ、キサントモナス・オリザエ 病原型オリジコーラ及びキサントモナス・シトリ 病原型シトリ、からなる群から選択される。第3の点において、病原性E.アミロボーラは、ストレプトマイシン耐性E.アミロボーラである。第4の点において、作物は、バナナ、リンゴ、ナシ、クラブアップル、柑橘類、ジャガイモ、カボチャ、タマネギ、コメ、アフリカスミレ;ニンジン、ジャガイモ、トマト、ナス、葉菜類、スカッシュ及びカボチャウリ類などのアブラナ科、ナス科、ウリ科の植物種、コショウ及びグリーンペッパー、オリーブ;オリーブ、モモ、クルミを含む石果及びナシ状果植物、の1つ以上から選択される。第5の点において、病原性細菌は、フラボバクテリウム・コルムナーレ(Flavobacterium columnare)#2、フラボバクテリウム・コルムナーレMS-FC-4である。第6の点において、病原性細菌は、E.コーライ(E.coli)O157:H7である。
In the first respect, the crop disease is selected from the group consisting of fire blight, citrus carcinoma, olive carcinoma, soft rot, tomato and pepper. In the second respect, pathogenic microorganisms include Mycospherella fisiensis, Botrytis cinerea, Erwinia amylovora (Ea) (particularly streptomycin-resistant E. amylovora strains), Xanthomonas axonopodis pathovar citri (Xac), Pectobacterium pallidum. Mentieri, Pectobacterium atrosepticum, Pectobacterium carotovorum subspecies brasiliensis, Pectobacterium carotovorum subspecies carotovorum, Dikeya dadantii, Pseudomonas savastanoi (Psv), Pseudomonas syringae pathogenic type tomato, Pseudomonas syringae Pathotype syringae, Pseudomonas syringae Pathotype lacrimans, Xanthomonas campestris Pathotype purni, Xanthomonas campestris Pathotype Vesicatoria, Xanthomonas arboricola Pathotype jugrandis, Ralstonia solanacearum, Clavibacter michiganensis species Michiganensis, Phytophthora infestans, Venturia inaecualis, Xanthomonas oryzae, Xanthomonas oryzae, Xanthomonas orygicola, and Xanthomonas citri, Xanthomonas oryzae. In the third point, pathogenic E. Amylovora is a streptomycin-resistant E. It is Amylovora. In the fourth respect, the crops are cruciferous, such as bananas, apples, pears, crabapples, citrus fruits, potatoes, pumpkins, onions, rice, African violets; carrots, potatoes, tomatoes, eggplants, leafy vegetables, squash and cucurbits; , Solanaceae, Cucurbitaceae, peppers and green peppers, olives; stone fruit and pome fruit plants, including olives, peaches, and walnuts. In the fifth point, the pathogenic bacteria are
第8の態様において、結晶性化合物は、以下の構造の1つから選択される。 In an eighth aspect, the crystalline compound is selected from one of the following structures.
第1の点において、結晶性化合物は、以下の構造であり、 In the first point, the crystalline compound has the following structure:
第2の点において、結晶性化合物は、以下の構造であり、 In the second point, the crystalline compound has the following structure:
第3の点において、結晶性化合物は、以下の構造であり、 In the third point, the crystalline compound has the following structure:
生物寄託情報
細菌株シュードモナス・ソリ 0617-T307、シュードモナス・ソリ 0917-T305、シュードモナス・ソリ 0917-T306、シュードモナス・ソリ 0917-T307、シュードモナス・モッセリイ 0118-T319、シュードモナス・モッセリイ 0318-T327、及びシュードモナス・モッセリイ 0418-T328がAmerican Type Culture Collection(ATCC(登録商標))、P.O. Box 1549、 Manassas、VA 20110 USA(「ATCC特許寄託機構」)に2020年6月25日に提出され、それぞれ非公式ATCC特許番号PTA-126796、PTA-126797、PTA-126798、PTA-126799、PTA-126800、PTA-126801、及びPTA-126802を付与された。生存率試験後、ATCC特許寄託機構は、これらの寄託された細菌株に、2020年6月25日から有効な以下の受託番号を付与した:シュードモナス・ソリ 0617-T307(受託番号PTA-126796)、シュードモナス・ソリ 0917-T305(受託番号PTA-126797)、シュードモナス・ソリ 0917-T306(受託番号PTA-126798)、シュードモナス・ソリ 0917-T307(受託番号PTA-126799)、シュードモナス・モッセリイ 0118-T319(受託番号PTA-126800)、シュードモナス・モッセリイ 0318-T327(受託番号PTA-126801)及びシュードモナス・モッセリイ 0418-T328(受託番号PTA-126802)。
Biological deposits bacterial stocks Monas Soli 0617 -T307, Subu Monas Soli 0917 -T305, Subu Monas Soli 0917 -T306, Subu Demonas Soli 0917 -T307, Subu Demonas Mosceri 0118 -T319, Subud Monas Monas 0318 -T327, and Sched Monas Mosseri 0418-T328 is available from the American Type Culture Collection (ATCC (registered trademark)), P.M. O. Box 1549, Manassas, VA 20110 USA (the "ATCC Patent Depositary") on June 25, 2020, and unofficial ATCC Patent Numbers PTA-126796, PTA-126797, PTA-126798, PTA-126799, PTA, respectively. -126800, PTA-126801, and PTA-126802. After viability testing, the ATCC Patent depository has assigned these deposited bacterial strains the following accession number, effective June 25, 2020: Pseudomonas sori 0617-T307 (Accession number PTA-126796) , Pseudomonas sori 0917-T305 (accession number PTA-126797), Pseudomonas sori 0917-T306 (accession number PTA-126798), Pseudomonas sori 0917-T307 (accession number PTA-126799), Pseudomonas mosselii 0118-T319 ( Accession number PTA-126800), Pseudomonas mosselii 0318-T327 (Accession number PTA-126801), and Pseudomonas mosseri 0418-T328 (Accession number PTA-126802).
[実施例1] 0617-T307菌株の同定及び特徴付け [Example 1] Identification and characterization of strain 0617-T307
16S rDNA、gyrB、rpoB、rpoDの部分配列が解析された。これらの4つの遺伝子は、シュードモナス属の多座配列解析(MLSA)の推奨マーカーである(Peixら、(2018))。 Partial sequences of 16S rDNA, gyrB, rpoB, and rpoD were analyzed. These four genes are recommended markers for multilocus sequence analysis (MLSA) of Pseudomonas (Peix et al. (2018)).
種の帰属のために、これらの4つの配列を使用して、NCBI非冗長ヌクレオチドデータベースに対してBLASTNを実行した。結果に基づき、0617-T307菌株はP.フルオレッセンス系統のP.プチダ群に属するシュードモナス属種に近縁である。「MLSA系統樹」及び「シュードモナス属種の標準菌株由来のゲノムリスト」(Peixら、(2018);Peixら、(2018)の図2及び表2参照)を分類サンプリングのガイドとして用いた(図1)。この情報をもとに、GenBankからゲノムを取得した。高品質なゲノムアセンブリを持つP.プチダ群のすべての種が含まれた。0617-T307はP.ソリと最も高いrpoD(すなわち、シュードモナス属種の割り当てに最も高い解像力を持つ遺伝子)配列類似性を持つため、P.ソリの利用可能な4種類のゲノムすべてをサンプリングに含めた(P.soliの標準菌株LMG 27941Tを含む)。P.フルオレッセンス系統の他の種については、それぞれのグループの代表として1種を選択した。P.エルジノーサ(P.エルジノーサ群、P.エルジノーサ系統)は、ツリーのルートを作成するためのアウトグループとして含まれた。 For species assignment, these four sequences were used to run BLASTN against the NCBI non-redundant nucleotide database. Based on the results, strain 0617-T307 is P. Fluorescens strain P. It is closely related to Pseudomonas species belonging to the group Putida. The “MLSA phylogenetic tree” and the “genome list derived from standard strains of Pseudomonas species” (Peix et al., (2018); see Figure 2 and Table 2 of Peix et al., (2018)) were used as a guide for taxonomic sampling (Fig. 1). Based on this information, the genome was obtained from GenBank. P. with a high-quality genome assembly. All species of the Putida group were included. 0617-T307 is P. Because it has the highest rpoD (i.e., the gene with the highest resolution for Pseudomonas species assignment) sequence similarity to P. All four available genomes of P. soli were included in the sampling (including the standard strain of P. soli LMG 27941 T ). P. For other species of the fluorescens lineage, one species was selected as a representative of each group. P. P. aeruginosa (P. aeruginosa group, P. aeruginosa lineage) was included as an outgroup to create the root of the tree.
MLSA用の4つの遺伝子は、サンプリングされたゲノムから抽出された。それぞれの遺伝子が個別に配列された後、系統解析のために4つのヌクレオチドアライメントがすべて連鎖された。連鎖されたアライメントは、9,912個の配列されたヌクレオチド部位が含まれる。最尤推定はPhyML(Guindonら、(2003))を用いて行われた。ブートストラップ支持は1,000個の複製によって評価された。 Four genes for MLSA were extracted from the sampled genome. After each gene was sequenced individually, all four nucleotide alignments were linked together for phylogenetic analysis. The linked alignment includes 9,912 aligned nucleotide sites. Maximum likelihood estimation was performed using PhyML (Guindon et al. (2003)). Bootstrap support was estimated by 1,000 replicates.
多座分子系統樹(図1)に基づき、0617-T307及びゲノム配列が利用可能な4つのP.ソリ菌株は、100%のブートストラップ支持で単系統クレードを形成する。この結果は、0617-T307を、スペインのシエラネバダ国立公園の土壌試料から分離されたことが報告されている標準菌株であるP.ソリ(Pascualら、(2014))に割り当てる強い裏付けを提供した。 Based on the multilocus molecular phylogenetic tree (Figure 1), 0617-T307 and the four P. elegans for which genome sequences are available. The Soli strains form a monophyletic clade with 100% bootstrap support. This result indicates that 0617-T307 is a standard strain of P. spp. that has been reported to be isolated from soil samples in Sierra Nevada National Park, Spain. provided strong support for assigning it to Soli (Pascual et al., (2014)).
さらに、Garcia-Valdes及びLalucatによって提供されたシュードモナス属種割り当てのためのガイドライン((Garcia-Valdesら、(2016))に基づき、0617-T307をP.ソリに割り当てるための追加の支持は、以下を含めた。(a)16S rDNA>98.7~99%同一。P.ソリの標準菌株と比較して、0617-T307は99.2%の配列同一性を有していた。姉妹種であるP.エントモフィラ(P.entomophila)と比較すると、0617-T307は99.5%の配列同一性を有していた。16S rDNAはシュードモナス属における種同定に十分な解像力がないことが知られていることに注意されたい(Garcia-Valdesら、(2016);Peixら、(2018));(b)rpoD遺伝子>95~96%同一。P.ソリの標準菌株と比較して、0617-T307は96.5%の配列同一性を有していた。姉妹種であるP.エントモフィラと比較して、0617-T307は89.1%の配列同一性しか有さなかった;及び(c)MLSA>97%同一。P.ソリの標準菌株と比較して、0617-T307は98.0%の配列同一性を有していた。姉妹種であるP.エントモフィラと比較すると、0617-T307は95.1%の配列同一性しか有さなかった。 Additionally, based on the guidelines for Pseudomonas species assignment provided by Garcia-Valdes and Lalucat ((Garcia-Valdes et al., (2016)), additional support for assigning 0617-T307 to P. sori is provided below. (a) 16S rDNA>98.7-99% identical. Compared to the standard strain of P. sori, 0617-T307 had 99.2% sequence identity. When compared to P. entomophila, 0617-T307 had 99.5% sequence identity. 16S rDNA is known to lack sufficient resolution for species identification in the genus Pseudomonas. Note that (Garcia-Valdes et al., (2016); Peix et al., (2018)); (b) rpoD gene >95-96% identical. 0617- T307 had 96.5% sequence identity. Compared to its sister species P. entomophila, 0617-T307 had only 89.1% sequence identity; and (c ) MLSA>97% identical. Compared to the standard strain of P. sori, 0617-T307 had 98.0% sequence identity. Compared to its sister species, P. entomophila, 0617-T307 had 98.0% sequence identity. T307 had only 95.1% sequence identity.
[実施例2] 0617-T307菌株の細胞ブロスの酢酸エチル抽出物由来のRejuAgro A及びRejuAgro Bの調製、単離、及び特徴付け Example 2 Preparation, isolation, and characterization of RejuAgro A and RejuAgro B from ethyl acetate extract of cell broth of strain 0617-T307
RejuAgro A及びBの調製は、発酵槽発酵の細胞ブロスを酢酸エチル抽出し、その後クロマトグラフィーで単離及び精製することにより得ることができる。簡単に説明すると、ストック細菌であるシュードモナス属種0617-T307をLBプレート(10g/L トリプトン、5g/L 酵母エキス、10g/L NaCl、15g/L 寒天、水)に画線塗布し、28℃のインキュベーター内で24時間増殖させた。種培地の調製においては、0617-T307の単一コロニーを、500mLのオートクレーブしたYME培地(4g/L 酵母エキス、4g/L グルコース、10g/L 麦芽エキス)を含む2.0Lフラスコに接種し、28℃で200rpmの振盪速度で24時間増殖させる。次いで、12LのオートクレーブしたYME培地を含む20LのNBS発酵槽に種培地を接種した。発酵は16℃で1~7日間進行させた。撹拌速度は200rpm、送風量は2L/分であった。 The preparation of RejuAgro A and B can be obtained by ethyl acetate extraction of the cell broth of the fermentor fermentation followed by chromatographic isolation and purification. Briefly, stock bacteria Pseudomonas sp. 0617-T307 were streaked onto LB plates (10 g/L tryptone, 5 g/L yeast extract, 10 g/L NaCl, 15 g/L agar, water) and incubated at 28°C. The cells were grown for 24 hours in an incubator. For seed medium preparation, a single colony of 0617-T307 was inoculated into a 2.0 L flask containing 500 mL of autoclaved YME medium (4 g/L yeast extract, 4 g/L glucose, 10 g/L malt extract); Grow for 24 hours at 28°C with a shaking speed of 200 rpm. A 20 L NBS fermentor containing 12 L of autoclaved YME medium was then inoculated with the seed medium. Fermentation proceeded for 1-7 days at 16°C. The stirring speed was 200 rpm, and the air flow rate was 2 L/min.
採取後、菌体培養物は酢酸エチルにより4回抽出された。酢酸エチル層が分離され、硫酸ナトリウムを用いて脱水した後、35℃でロータリーエバポレーションにより乾燥させた。この結果、0617-T307菌株の12L培養物から2.9gの粗抽出物が得られた。 After collection, the bacterial culture was extracted four times with ethyl acetate. The ethyl acetate layer was separated, dried with sodium sulfate, and then dried by rotary evaporation at 35°C. As a result, 2.9 g of crude extract was obtained from a 12 L culture of strain 0617-T307.
濃縮した試料は酢酸エチルに溶解され、シリカゲルと混合されてインジェクションカラム(φ3.0×20cm)として充填され、UV検出器を備えたフラッシュクロマトグラフィーシステム(Yamazen AI-580)のシリカゲルユニバーサルカラム(4.8×18.5cm)の上に装填された。試料を装填した後、試料は、極性が増加する順に、100%ヘキサン、75%ヘキサン/25%酢酸エチル、50%ヘキサン/50%酢酸エチル、25%ヘキサン/75%酢酸エチル、100%酢酸エチル、50%酢酸エチル/50%アセトン、100%アセトン、及び100%メタノールのそれぞれの溶媒280mLによって溶出された。試料は20mL/分の流速で溶出された。溶出液はUV254nmでモニターされ、フラクションは20mL/試験管の時間モードにより回収された。フラッシュクロマトグラフィーから得られたフラクション又は試験管は合計114本であった。 The concentrated sample was dissolved in ethyl acetate, mixed with silica gel and packed as an injection column (φ 3.0 × 20 cm), and placed in a silica gel universal column (4) of a flash chromatography system (Yamazen AI-580) equipped with a UV detector. .8 x 18.5 cm). After loading the samples, the samples were tested in order of increasing polarity: 100% hexane, 75% hexane/25% ethyl acetate, 50% hexane/50% ethyl acetate, 25% hexane/75% ethyl acetate, 100% ethyl acetate. , 50% ethyl acetate/50% acetone, 100% acetone, and 100% methanol. Samples were eluted at a flow rate of 20 mL/min. The eluate was monitored by UV 254 nm and fractions were collected by time mode at 20 mL/tube. A total of 114 fractions or test tubes were obtained from flash chromatography.
生成されたフラクションは、その後のプレートアッセイに適用された。それぞれのフラクションの1mLを1.5mL試験管に採取し、エッペンドルフ真空濃縮機で真空乾燥させた。乾燥された試料は、50μLのDMSOに溶解され、そのうちの2μLがプレートアッセイに使用された。簡単に説明すると、エルウィニア・アミロボーラ273を、LBプレートに画線塗布して28℃のインキュベーター内で増殖させ、24時間後に得られた単一コロニーを5mLのLB培地に接種して28℃、200rpmの振盪機で一晩増殖させた。菌体を滅菌水で1:100に希釈し、そのうちの225μLを50%LBプレート(5.0g/L トリプトン、2.5g/L 酵母エキス、5.0g/L NaCl、15g/L 寒天)上にプレーティングした。バイオセーフティキャビネット内で10分間乾燥させた後、それぞれのフラクションのDMSO溶液をシャーレのあらかじめラベルを貼った部分に分配し、さらに10分間乾燥させた。アッセイに伴い、DMSO及びカスガマイシンをそれぞれ陰性対照及び陽性対照として使用した。次いで、プレートは28℃のインキュベーターでインキュベートされ、1日後に阻止円が確認された。 The generated fractions were applied to subsequent plate assays. 1 mL of each fraction was collected in a 1.5 mL test tube and vacuum dried in an Eppendorf vacuum concentrator. The dried sample was dissolved in 50 μL of DMSO, of which 2 μL was used for plate assay. Briefly, Erwinia amylovora 273 was streaked onto an LB plate and grown in an incubator at 28°C, and after 24 hours, a single colony obtained was inoculated into 5 mL of LB medium and incubated at 28°C and 200 rpm. Grow overnight on a shaker. The bacterial cells were diluted 1:100 with sterile water, and 225 μL of it was placed on a 50% LB plate (5.0 g/L tryptone, 2.5 g/L yeast extract, 5.0 g/L NaCl, 15 g/L agar). Plated. After drying in a biosafety cabinet for 10 minutes, the DMSO solution of each fraction was dispensed onto a pre-labeled area of the Petri dish and allowed to dry for an additional 10 minutes. Along with the assay, DMSO and kasugamycin were used as negative and positive controls, respectively. The plates were then incubated in a 28°C incubator, and inhibition zones were observed after 1 day.
114フラクションのインビトロプレートアッセイでは、E.アミロボーラ273の増殖を抑制するフラクションが2つ示された。特筆すべきは、フラクション/試験管38~40(これは、T3840又はFlash-RejuAgro Aと略記された)は50%ヘキサン/50%酢酸エチルによって溶出され、さらなる試験で有望となり得る比較的大きなクリアランスゾーンを有していた。このアッセイにおける他の生物活性化合物は、フラクション50~52(これはT5052としてコード化された)にあった。これらのフラクションは、25%ヘキサン/75%酢酸エチルによって溶出された。 In an in vitro plate assay of 114 fractions, E. Two fractions were shown to inhibit the proliferation of Amylobora 273. Notably, fraction/tube 38-40 (which was abbreviated as T3840 or Flash-RejuAgro A) was eluted with 50% hexane/50% ethyl acetate, showing a relatively large clearance that may be promising for further testing. It had a zone. The other bioactive compound in this assay was in fractions 50-52 (which was coded as T5052). These fractions were eluted with 25% hexane/75% ethyl acetate.
フラクション3840及び5054を分取HPLC(Prep-HPLC)で精製した結果、黄色に着色した化合物RejuAgro A(Rt17.5)15mgと暗緑色に着色した化合物RejuAgro B103.3mgをそれぞれ発見した。RejuAgro Aは、メタノール及びクロロホルムに溶解され得る。RejuAgro B(Rt10.5)はメタノール及びクロロホルムには十分に溶解されないが、ジメチルスルホキシド(DMSO)には非常によく溶解され、濃緑色を呈する。この2つの化合物の構造を、高分解能質量分析(HR-MS)、赤外線(IR)、紫外線(UV)、1次元及び2次元核磁気共鳴(NMR)、X線結晶構造解析によって調べた。その結果、この2つの化合物は構造的に類似しており、化合物RejuAgro Aは7種類の炭素基(3種類のカルボニル基、2種類の3級炭素、2種類のメチル炭素)を有するが、RejuAgro Bは以下に示すように1種類のメチル基を欠いている: As a result of purifying fractions 3840 and 5054 by preparative HPLC (Prep-HPLC), 15 mg of a yellow colored compound RejuAgro A (Rt17.5) and 103.3 mg of a dark green colored compound RejuAgro B were discovered, respectively. RejuAgro A can be dissolved in methanol and chloroform. RejuAgro B (Rt10.5) is not well soluble in methanol and chloroform, but is very well soluble in dimethyl sulfoxide (DMSO) and has a dark green color. The structures of these two compounds were investigated by high-resolution mass spectrometry (HR-MS), infrared (IR), ultraviolet (UV), one-dimensional and two-dimensional nuclear magnetic resonance (NMR), and X-ray crystallography. As a result, the two compounds are structurally similar, and the compound RejuAgro A has seven types of carbon groups (three types of carbonyl groups, two types of tertiary carbons, and two types of methyl carbons), whereas RejuAgro A has seven types of carbon groups (three types of carbonyl groups, two types of tertiary carbons, and two types of methyl carbons). B lacks one methyl group as shown below:
さらに、そのクロロホルム溶液を室温でゆっくり蒸発させることにより、RejuAgro Aの結晶が得られた。この結晶はオレンジ色の板状小片として同定された。データセットは、Cu(Kα)放射を用いたOxford SuperNova回折計で100Kで収集された。この分子は平面構造をしており、S-Me(メチル)基は複素環に対して8.7°だけ回転している。この分子では、C4-C5結合(1.531Å)で顕著なπ共役の切断が見られるが、これは明らかに何らかの軌道上の理由がある。sp2の炭素原子に接続するMe基は、2つの位置で回転的に無秩序である。結晶中の分子は、N-H...O相互作用によって中心対称なH結合二量体を形成する。さらに、これらの二量体は、より弱いC-H...O相互作用を介して[-3 0 1]面に沿って2次元層を形成する。RejuAgro A分子は、6員複素環[-NH-C(=O)-C(-SMe)=C(-Me)-C(=O)-C(=O)-]を示す。RejuAgro Bの結晶は三斜晶として同定された。RejuAgro Bの構造は、対称的に独立した2つの分子を含む。それぞれの分子はねじれた構造をしており、連結した複素環の平均面間の二面角は70.3°及び80.6°である。それぞれのヘテロ環には、隣接する2つのカルボニル基間のC(sp2)-C(sp2)結合で顕著なπ共役の切断が見られるが(結合長は1.534~1.539Åの範囲)、これは明らかに何らかの軌道上の理由がある。結晶中の分子は、N-H...O相互作用によって中心対称なH-結合二量体を形成する。これらの二量体は、他のN-H...O相互作用によってx方向に沿って積重して連結される。最後に、積み重なりは、3種類目のN-H...O相互作用によって、[0 1 1]方向に沿って層状に連結される。RejuAgro B溶液を結晶成長に使用した場合、2つの結晶が得られ、RejuAgro B及びRejuAgro Cと命名された。RejuAgro B及びRejuAgro Cの両方の結晶は、非常に類似した分子量を有している(実施例20参照)。 Furthermore, crystals of RejuAgro A were obtained by slowly evaporating the chloroform solution at room temperature. The crystals were identified as orange plate-like pieces. Data sets were collected at 100K on an Oxford SuperNova diffractometer using Cu (Kα) radiation. This molecule has a planar structure, with the S-Me (methyl) group rotated by 8.7° relative to the heterocycle. This molecule shows significant π-conjugation cleavage at the C4-C5 bond (1.531 Å), which clearly has some orbital reason. The Me group attached to the sp 2 carbon atom is rotationally disordered in two positions. The molecules in the crystal are NH. .. .. A centrosymmetric H-bond dimer is formed by O interaction. Furthermore, these dimers have a weaker C-H. .. .. A two-dimensional layer is formed along the [-3 0 1] plane through O interaction. The RejuAgro A molecule exhibits a 6-membered heterocycle [-NH-C(=O)-C(-SMe)=C(-Me)-C(=O)-C(=O)-]. The crystals of RejuAgro B were identified as triclinic. The structure of RejuAgro B includes two symmetrically independent molecules. Each molecule has a twisted structure, and the dihedral angles between the average planes of the connected heterocycles are 70.3° and 80.6°. In each heterocycle, significant π-conjugation cleavage is observed at the C(sp 2 )-C(sp 2 ) bond between two adjacent carbonyl groups (bond length is 1.534-1.539 Å). range), there is clearly some orbital reason for this. The molecules in the crystal are NH. .. .. A centrosymmetric H-bond dimer is formed by O interaction. These dimers are similar to other N-H. .. .. They are stacked and connected along the x direction by O interaction. Finally, the stack is the third type of N-H. .. .. Due to the O interaction, they are connected in a layered manner along the [0 1 1] direction. When RejuAgro B solution was used for crystal growth, two crystals were obtained and named RejuAgro B and RejuAgro C. Both RejuAgro B and RejuAgro C crystals have very similar molecular weights (see Example 20).
RejuAgro A、RejuAgro B、及びRejuAgro Cの結晶構造情報は、実施例20に示されており、その内容は本願の一部を構成し、その全体を参照により組み込む。 Crystal structure information for RejuAgro A, RejuAgro B, and RejuAgro C is provided in Example 20, the contents of which constitute a part of this application and are incorporated by reference in its entirety.
RejuAgro Aの分子式はC7H7NO3Sであり、分子量:185.2004である。これは、HR-MSデータで観測された[M+H]の分子種m/z186.2177(理論値186.2083)と一致する。RejuAgro Bの分子式はC12H8N2O6Sであり、分子量:276.2017である。これは、HR-MSデータで観測された[M-H]の分子種m/z275.0278(理論値275.1960)と一致する。2020年8月4日時点のCCDC構造データベース検索は、RejuAgro A、RejuAgro B、及びRejuAgro Cの結晶構造は存在しないことを示唆する。SciFinder、Reaxys、Google特許及び特許関連データベース検索などの他の化学データベースでは、SciFinder及びReaxysからRejuAgro Bに関する1件の文献(Knackmussら、(1968))が見つかった以外はRejuAgro A又はRejuAgro Cの類似体は存在しないことが示された。 The molecular formula of RejuAgro A is C 7 H 7 NO 3 S, and the molecular weight is 185.2004. This agrees with the molecular species m/z of [M+H] observed in HR-MS data, m/z 186.2177 (theoretical value 186.2083). The molecular formula of RejuAgro B is C 12 H 8 N 2 O 6 S, and the molecular weight is 276.2017. This agrees with the molecular species m/z of [MH] observed in HR-MS data, m/z 275.0278 (theoretical value 275.1960). CCDC structure database search as of August 4, 2020 suggests that crystal structures for RejuAgro A, RejuAgro B, and RejuAgro C do not exist. Other chemical databases such as SciFinder, Reaxys, Google Patent and Patent Related Database Searches showed no similarity to RejuAgro A or RejuAgro C except for one publication (Knackmuss et al., (1968)) for RejuAgro B from SciFinder and Reaxys. The body was shown not to exist.
[実施例3] 0617-T307菌株由来のRejuAgro A及びRejuAgro Bのインビトロ抗菌活性 [Example 3] In vitro antibacterial activity of RejuAgro A and RejuAgro B derived from strain 0617-T307
野生型グラム陰性植物病原性細菌、ストレプトマイシン耐性E.アミロボーラ、魚病原因細菌、グラム陽性及びグラム陰性ヒト病原性細菌、RejuAgro Aの生産菌(0617-T307菌株)の5種類の細菌に対して、RejuAgro A及びRejuAgro BのMIC値は決定された。抗菌性アッセイは、CLSI抗菌物質感受性テスト(AST)標準に準拠して実施された。簡単に説明すると、試験したそれぞれの菌のストック溶液をLB(Luria-Bertani)プレート(10g/L トリプトン、5g/L 酵母エキス、10g/L ナトリウム塩、15g/L 寒天)に画線塗布した。特殊培養では、NA(栄養ブロス+寒天)プレート(3g/L ビーフエキス、1g/L 酵母エキス、5g/L ポリペプトン、10g/L スクロース、15g/L 寒天)がXacに対して使用された。SHIEH(5g/L トリプトン、0.5g/L 酵母エキス、0.01g/L 酢酸ナトリウム、0.01g/L BaCl2(H2O)2、0.1g/L K2HPO4、0.05g/L KH2PO4、0.3g/L MgSO4・7H2O、0.0067g/L CaCl2・2H2O、0.001g/L FeSO4・7H2O、0.05g/L NaHCO3、10g/L 寒天)、及びTYES(4g/L トリプトン、0.4g/L 酵母エキス、0.5g/L MgSO4、0.5g/L CaCl2、pH7.2、15g/L 寒天)がそれぞれフラボバクテリウム・コルムナーレ菌株MS-FC-4及び#2に対して使用された。その後、プレートから単一コロニーを拾い上げ、対応する液体培地に接種して一晩増殖させた。この培養物はLB又は対応する培地でOD590=0.01に希釈され、96ウェルプレートに200μL/ウェルで分配された。化合物RejuAgro A及びRejuAgro B及びストレプトマイシンは希釈され、それぞれの濃度の4μLがそれぞれのウェルに添加され、最終濃度は40μg/mL、20μg/mL、10μg/mL、5μg/mL、2.5μg/mL、1.25μg/mL、0.625μg/mL、0.3125μg/mL、0.15625μg/mL、0.078μg/mLとする。対照として、ビヒクル水(ストレプトマイシンの場合)又はDMSO(RejuAgro A及びRejuAgro Bの場合)を使用した。 A wild-type Gram-negative phytopathogenic bacterium, streptomycin-resistant E. The MIC values of RejuAgro A and RejuAgro B were determined for five types of bacteria: Amylobora, fish disease-causing bacteria, Gram-positive and Gram-negative human pathogenic bacteria, and the producer of RejuAgro A (strain 0617-T307). Antimicrobial assays were performed according to CLSI Antimicrobial Susceptibility Testing (AST) standards. Briefly, stock solutions of each fungus tested were streaked onto LB (Luria-Bertani) plates (10 g/L tryptone, 5 g/L yeast extract, 10 g/L sodium salts, 15 g/L agar). For special culture, NA (nutrient broth + agar) plates (3 g/L beef extract, 1 g/L yeast extract, 5 g/L polypeptone, 10 g/L sucrose, 15 g/L agar) were used for Xac. SHIEH (5g/L tryptone, 0.5g/L yeast extract, 0.01g/L sodium acetate, 0.01g/L BaCl2 ( H2O ) 2 , 0.1g /L K2HPO4 , 0.05g /L KH2PO4 , 0.3g / L MgSO4.7H2O , 0.0067g/L CaCl2.2H2O , 0.001g /L FeSO4.7H2O , 0.05g /L NaHCO3 , 10 g/L agar), and TYES (4 g/L tryptone, 0.4 g/L yeast extract, 0.5 g/L MgSO4, 0.5 g/L CaCl 2 , pH 7.2, 15 g/L agar), respectively. It was used against Bacterium columunale strains MS-FC-4 and #2. A single colony was then picked from the plate and inoculated into the corresponding liquid medium and grown overnight. This culture was diluted with LB or the corresponding medium to OD 590 =0.01 and distributed in 96-well plates at 200 μL/well. Compounds RejuAgro A and RejuAgro B and streptomycin were diluted and 4 μL of each concentration was added to each well, with final concentrations of 40 μg/mL, 20 μg/mL, 10 μg/mL, 5 μg/mL, 2.5 μg/mL, 1.25 μg/mL, 0.625 μg/mL, 0.3125 μg/mL, 0.15625 μg/mL, and 0.078 μg/mL. Vehicle water (for streptomycin) or DMSO (for RejuAgro A and RejuAgro B) was used as a control.
アッセイの結果は、0617-T307菌株の最も活性な代謝物は、RejuAgro BではなくRejuAgro Aであることを示した。グラム陽性菌のMRSA(MIC>40μg/mL)及びグラム陰性菌のE.コーライO157:H7(ヒトに下痢、出血性大腸炎、溶血性尿毒症症候群(HUS)を引き起こす食品及び水媒介性重要病原菌)(MIC=40μg/mL)に対する効果と比較すると、RejuAgro AはMIC値が5~40μg/mLの試験細菌に対して特に効率的である。RejuAgro Aの抗菌活性は、エルウィニア・アミロボーラ 1189、キサントモナス・アキソノポディス 病原型シトリ、シュードモナス・サバスタノイ 病原型サバスタノイ、ペクトバクテリウム・パルメンティエリ UPP163 936、ペクトバクテリウム・カロトボラム 亜種ブラシリエンシス 944、ペクトバクテリウム・カロトボラム 亜種カロトボラム wpp14 945、ディケヤー・ダダンティイ 3937菌株に関してはストレプトマイシンと同等であり、E.アミロボーラに関するMIC値は5μg/mLであり、他の弱い病原性細菌では20~40μg/mLであった。キサントモナス細菌はストレプトマイシに対して非常に感受性が高く、MIC値は0.16μg/mLで、これはRejuAgro Aに対するMIC値5μg/mLより低い。シュードモナス・サバスタノイ 病原型サバスタノイに対するRejuAgro AのMIC値は40μg/mLである。キサントモナス・アルボリコーラ 病原型ジュグランディス219に対するRejuAgro AのMIC値は6.25μg/mLである。ラルストニア・ソラナセアラム K60及びPss4に対するRejuAgro AのMIC値は、それぞれ3.13及び6.25μg/mLである。クラビバクター・ミシガンエンシス 亜種ミシガンエンシス NCPPB382、Cmm0317、Cmm0690に対するRejuAgro AのMIC値はそれぞれ6.25、1.56、12.5μg/mLである。ラルストニア・ソラナセアラム K60及びPss4に対するRejuAgro AのMIC値は40μg/mLである。 The assay results showed that the most active metabolite of strain 0617-T307 was RejuAgro A rather than RejuAgro B. Gram-positive bacteria MRSA (MIC>40 μg/mL) and Gram-negative bacteria E. RejuAgro A has a MIC value of 40 μg/mL when compared to its efficacy against K. coli O157:H7 (an important food- and water-borne pathogen that causes diarrhea, hemorrhagic colitis, and hemolytic uremic syndrome (HUS) in humans) (MIC = 40 μg/mL). It is particularly efficient against test bacteria of 5-40 μg/mL. The antibacterial activity of RejuAgro A was shown to be against Erwinia amylovora 1189, Xanthomonas axonopodis pathotype citri, Pseudomonas savastanoi pathotype sabastanoi, Pectobacterium palmentieri UPP163 936, Pectobacterium carotovorum subsp. brasiliensis 944, Pectobacterium E. carotovorum subspecies carotovorum wpp14 945 and D. dadantii 3937 strains are equivalent to streptomycin; The MIC value for Amylobora was 5 μg/mL and for other weakly pathogenic bacteria 20-40 μg/mL. Xanthomonas bacteria are highly susceptible to Streptomyces with a MIC value of 0.16 μg/mL, which is lower than the MIC value for RejuAgro A of 5 μg/mL. The MIC value of RejuAgro A against Pseudomonas savastanoi pathotype is 40 μg/mL. The MIC value of RejuAgro A against Xanthomonas arboricola pathotype Jugrandis 219 is 6.25 μg/mL. The MIC values of RejuAgro A against Ralstonia solanacearum K60 and Pss4 are 3.13 and 6.25 μg/mL, respectively. The MIC values of RejuAgro A for Clavibacter michiganensis subspecies michiganensis NCPPB382, Cmm0317, and Cmm0690 are 6.25, 1.56, and 12.5 μg/mL, respectively. The MIC value of RejuAgro A against Ralstonia solanacearum K60 and Pss4 is 40 μg/mL.
また、RejuAgro Aは、病原性E.アミロボーラ1菌株とストレプトマイシン耐性E.アミロボーラ3菌株を含む他のE.アミロボーラ菌株に対しても試験された。E.アミロボーラ 110に対して、RejuAgro Aはストレプトマイシンと同等の効果を示した(MIC値5μg/mL)。しかしながら、RejuAgro AはE.アミロボーラ 1189に対して,ストレプトマイシンよりも効果が高い。E.アミロボーラ 1189に対するRejuAgro A及びストレプトマイシンのMIC値は、それぞれ5μg/mL及び10μg/mLである。さらに、RejuAgro Aに対してストレプトマイシンのMIC値(40μg/mL超)よりも低いMIC値(10μg/mL)が観察されたため、ストレプトマイシン耐性E.アミロボーラ CA11、DM1及び898に対してはより効果的である。これらの結果は、RejuAgro AがE.アミロボーラに対するテストにおいて最も強力な化合物であり、ストレプトマイシンの代替候補となりうることを示唆する。ストレプトマイシン耐性株におけるRejuAgro Aに対する交差耐性の徴候はない。
In addition, RejuAgro A is a
魚類のカラムナリス病の原因菌であるフラボバクテリウムに対して、RejuAgro Aはフラボバクテリウム・コルムナーレ MS-FC-4菌株及び#2菌株(天然及び養殖魚のカラムナリス病を引き起こす)に対してMIC値5μg/mLであり、この値はストレプトマイシンのMIC値より高かった(#2菌株及びMS-FC-4菌株に対してそれぞれ0.31μg/mL及び1.25μg/mL)。
Regarding Flavobacterium, which is the causative agent of columnaris disease in fish, RejuAgro A has an MIC value of 5 μg against Flavobacterium columnarie MS-FC-4 strain and strain #2 (which causes columnaris disease in wild and farmed fish). /mL, which was higher than the MIC value of streptomycin (0.31 μg/mL and 1.25 μg/mL for
0617-T307菌株に対するRejuAgro Aの影響を検証した。シュードモナス・ソリ 0617-T307(RejuAgro A生産菌)に対するRejuAgro AのMIC値は、試験したLB培地において40μg/mLより大きいことが示され、このことは0617-T307菌株は少なくとも自ら生産した40μg/mLのRejuAgro Aに対して生存及び耐性を持つことを意味する。 The effect of RejuAgro A on the 0617-T307 strain was verified. The MIC value of RejuAgro A against Pseudomonas sori 0617-T307 (RejuAgro A-producing strain) was shown to be greater than 40 μg/mL in the tested LB medium, indicating that the 0617-T307 strain at least contained 40 μg/mL produced by itself. It means survival and resistance to RejuAgro A.
RejuAgro Aは、トマトの病原菌(P.シリンガエ 病原型トマト PT30、P.シリンガエ 病原型シリンガエ 7046、P.シリンガエ 病原型ラクリマンス 1188-1)及びその他の柑橘類がん腫病病原菌(キサントモナス・キャンペストリス 病原型プルニ、キサントモナス・キャンペストリス 病原型ベシカトリア XV-16)についてストレプトマイシンとともに試験された。P.シリンガエに対するRejuAgro AのMIC値は40μg/mL、ストレプトマイシンのMIC値は2.5~5μg/mLであった。X.キャンペストリス種に対しては、RejuAgro AのMIC値は2.5μg/mL又は40μg/mLであり、これは、ストレプトマイシンのMIC値20μg/mL又は40μg/mL超と比較して小さい。これらのことから、シュードモナス属を原因とするトマトの病原菌と比較した場合、キサントモナス・キャンペストリスの病原菌はストレプトマイシンよりもRejuAgro Aに対して感受性が高いことが示された。 RejuAgro A is a tomato pathogen (P. syringae tomato PT30, P. syringae 7046, P. syringae lacrimans 1188-1) and other citrus carcinoma disease pathogens (Xanthomonas campestris tomato). Pruni, Xanthomonas campestris (P. vesicatoria XV-16) was tested with streptomycin. P. The MIC value of RejuAgro A against S. syringae was 40 μg/mL, and the MIC value of streptomycin was 2.5 to 5 μg/mL. X. For Campestris species, the MIC value of RejuAgro A is 2.5 μg/mL or 40 μg/mL, which is small compared to the MIC value of streptomycin of 20 μg/mL or over 40 μg/mL. These results indicate that the pathogen of Xanthomonas campestris is more sensitive to RejuAgro A than to streptomycin when compared to the pathogen of tomato caused by the genus Pseudomonas.
RejuAgro Aは、試験したすべての病原性真菌に対して有効であった(表1)。RejuAgro Aは、フィトフトラ・インフェスタンス、ベンチュリア・イナエキュアリス、ミコスフェレラ・フィジエンシスに対して試験された。RejuAgro Aは、40μg/mL、80μg/mL、600μg/mLでP.インフェスタンス及びV.イナエキュアリスに対して100%の阻害を示した(表1)。 RejuAgro A was effective against all pathogenic fungi tested (Table 1). RejuAgro A was tested against Phytophthora infestans, Venturia inaequalis, and Mycospherella fisiensis. RejuAgro A has P. Infestans and V. It showed 100% inhibition against Ina equalis (Table 1).
[実施例4] 振盪フラスコ発酵における0617-T307菌株由来のRejuAgro Aの生産及び安定性 [Example 4] Production and stability of RejuAgro A derived from strain 0617-T307 in shake flask fermentation
RejuAgro Aの生産及び調製に用いる0617-T307の発酵は、振盪フラスコ発酵と発酵槽発酵の2つのアプローチで得ることができる。発酵槽発酵は、実施例2に記載した。本実施例では、フラスコ発酵は以下のように得ることができる。ストック細菌であるシュードモナス属種0617-T307を、YME寒天培地(4g/L 酵母エキス、4g/L グルコース、10g/L 麦芽エキス、15g/L 寒天)に画線塗布し、28℃のインキュベーターで24時間増殖させた。50mLの滅菌YME液体培地を含む250mLフラスコにおいて0617-T307の単一コロニーを16℃、220rpmで24時間増殖させることによって、種培地を作成した。次いで種培地を、4%の比率(v/v)で0.5L滅菌YME培地を含む4Lフラスコに接種した。2LのYME培地を含む8つの4Lフラスコへの接種(2%、v/v)に続いて、細菌は16℃で200~220rpmの振盪機で1~7日間増殖させた。 Fermentation of 0617-T307 used for the production and preparation of RejuAgro A can be obtained in two approaches: shake flask fermentation and fermentor fermentation. Fermenter fermentation was described in Example 2. In this example, flask fermentation can be obtained as follows. The stock bacteria Pseudomonas sp. 0617-T307 was streaked onto a YME agar medium (4 g/L yeast extract, 4 g/L glucose, 10 g/L malt extract, 15 g/L agar) and incubated in an incubator at 28°C for 24 hours. Grown for hours. Seed medium was made by growing a single colony of 0617-T307 for 24 hours at 16° C. and 220 rpm in a 250 mL flask containing 50 mL of sterile YME liquid medium. The seed medium was then inoculated into a 4L flask containing 0.5L sterile YME medium at a ratio of 4% (v/v). Following inoculation of eight 4L flasks containing 2L of YME medium (2%, v/v), bacteria were grown for 1-7 days at 16°C on a shaker at 200-220 rpm.
開発した標準曲線に従って、LC-MS分析によりRejuAgro Aの濃度が得られた。LC-MS分析用の試料の調製には、2つの方法が用いられた。1つのアプローチは、細胞ブロスを酢酸エチル(1mL:1mL、ボルテックス1分)で抽出し、遠心分離と酢酸エチル層の真空乾燥により酢酸エチル抽出物を得ることである。乾燥した酢酸エチル抽出物は40μLのメタノールに溶解され、2μLのメタノール溶液がLC-MS分析に使用された。もう1つの方法は、細胞ブロスを遠心分離して上清を得、次いでその上清と等量のメタノールを混合して50%メタノール溶液とし、そのうちの10μL溶液をLC-MSに注入する方法である。RejuAgro Aの生産は細胞外分泌であり、細胞内ではなく上清にRejuAgro Aが多く含まれていることが確認されたため、第2の方法を採用した(図3、パネルA)。
The concentration of RejuAgro A was obtained by LC-MS analysis according to the developed standard curve. Two methods were used to prepare samples for LC-MS analysis. One approach is to extract the cell broth with ethyl acetate (1 mL:1 mL,
7日間の発酵中、RejuAgro Aの総生産量は初日にピーク濃度に達し、その後、時間の増加とともに減少し始めた(図3、パネルB)。さらに、振盪フラスコ発酵において、6時間ごとにRejuAgro Aの生産量と細胞濃度について詳細な検討が行われた。RejuAgro Aの濃度(RejuAgro Aの総量)は18時間で最大値13.8mg/Lに達し、細菌細胞濃度は12時間で最大値2×1011CFU/mLに達し、このことはRejuAgro Aの生産が細胞の増殖に伴う生産プロセスであることが示された。 During the 7-day fermentation, the total production of RejuAgro A reached a peak concentration on the first day and then started to decrease with increasing time (Fig. 3, panel B). Furthermore, in the shake flask fermentation, detailed studies were conducted on the production amount and cell concentration of RejuAgro A every 6 hours. The concentration of RejuAgro A (total amount of RejuAgro A) reached a maximum value of 13.8 mg/L in 18 hours, and the bacterial cell concentration reached a maximum value of 2 × 10 11 CFU/mL in 12 hours, which indicates that the production of RejuAgro A was shown to be a production process associated with cell proliferation.
4Lの振盪フラスコ内の培地の体積は、RejuAgro Aの生産に影響を与える。YME培地を使用した4Lフラスコでは、500mLの体積サイズでのみRejuAgro Aの生産が確認され、1.0Lと1.5Lの体積サイズでは確認されなかった。この観察結果は、RejuAgro Aの生産が、高い通気状態に存在するのを好むことを示す。 The volume of medium in the 4L shake flask influences the production of RejuAgro A. In a 4L flask using YME medium, production of RejuAgro A was confirmed only in the volume size of 500 mL, and not in the volume sizes of 1.0 L and 1.5 L. This observation indicates that RejuAgro A production prefers to exist in high aeration conditions.
培地の種類と培養温度はRejuAgro Aの生産に影響を与える。LB培地はYME培地と並行して16℃又は28℃で試験された。RejuAgro Aの生産は、16℃においてYME培地では確認されたが、LB培地では確認されなかった。コロニー形成単位について、0617-T307菌株は16℃と28℃の両方のLB培地、及び28℃のYME培地で良好に増殖した。これらの結果は、RejuAgro Aの生産は培地特異的かつ温度依存的であることを示唆する。0617-T307由来の生産物に対する活性は、E.アミロボーラに対するプレートアッセイによってモニターされ、これはRejuAgro Aの生産と一致するものである。 The type of medium and culture temperature affect the production of RejuAgro A. LB medium was tested in parallel with YME medium at 16°C or 28°C. Production of RejuAgro A was confirmed in YME medium at 16°C, but not in LB medium. For colony forming units, strain 0617-T307 grew well in LB medium at both 16°C and 28°C, and in YME medium at 28°C. These results suggest that the production of RejuAgro A is medium specific and temperature dependent. Activity against products derived from E. 0617-T307 is This is consistent with RejuAgro A production, as monitored by plate assay for Amylobora.
RejuAgro Aの生産条件の適用性を確認するため、シュードモナス属 0617-T307菌株と並行して、他の10菌株のシュードモナス属も同条件で試験した。ハウスキーピング遺伝子の解析に従って、0917-T305、0917-T306、及び0917-T307はシュードモナス・ソリであると同定され、0118-T319、0318-T327、0418-T328はシュードモナス・モッセリイであると同定された。シュードモナス・ソリ及びシュードモナス・モッセリイの両方のタイプ菌株が報告されている(Daboussiら、(2002);Pascualら、(2014))。 In order to confirm the applicability of the production conditions of RejuAgro A, in parallel with the Pseudomonas 0617-T307 strain, 10 other Pseudomonas strains were also tested under the same conditions. According to housekeeping gene analysis, 0917-T305, 0917-T306, and 0917-T307 were identified as Pseudomonas sori, and 0118-T319, 0318-T327, and 0418-T328 were identified as Pseudomonas mosselii. . Both type strains of Pseudomonas sori and Pseudomonas mosselii have been reported (Daboussi et al. (2002); Pascual et al. (2014)).
0617-T307株とその系統的に近縁な種は、28℃、220rpmのYMEにおいてRejuAgro Aを生産できることが示された。この結果は、本方法が0617-T307株及びその近縁種の一部に対してRejuAgro Aを生産する特異性を有することを示唆する(表2)。0617-T307をYME培地で16℃、220rpmの振盪機で培養することによって得られた40時間の培養物についてLCMSで試験したところ、RejuAgro Aは室温で少なくとも4週間存在し、安定である。 It was shown that strain 0617-T307 and its closely related species can produce RejuAgro A at 28° C. and 220 rpm YME. This result suggests that this method has specificity for producing RejuAgro A for strain 0617-T307 and some of its related species (Table 2). RejuAgro A is present and stable at room temperature for at least 4 weeks as tested by LCMS on a 40 hour culture obtained by culturing 0617-T307 in YME medium at 16° C. on a shaker at 220 rpm.
[実施例5] 菌株0617-T307の細胞ブロスの、0617-T307及びE.アミロボーラに対する抗菌活性。 Example 5 Cell broth of strains 0617-T307 and E. Antibacterial activity against Amylobora.
0617-T307の細胞ブロス及び代謝物の抗菌試験には、2つのアッセイが使用された。1つはプレート拡散アッセイ、もう1つはマイクロプレートアッセイである。E.アミロボーラに対するRejuAgro A含有フラクション及び細胞ブロスの抗菌活性のプレート拡散アッセイには、LBプレートを使用した(表3)。0617-T307の生細胞を含む細胞ブロス及び2mg/mLのRejuAgro A含有懸濁液は、いずれもE.アミロボーラに対して抗菌活性を示した。しかし、Serenade(登録商標)を適用した場合には、阻止円は観察されなかった。 Two assays were used for antimicrobial testing of cell broth and metabolites of 0617-T307. One is a plate diffusion assay and the other is a microplate assay. E. LB plates were used for plate diffusion assays of the antibacterial activity of RejuAgro A-containing fractions and cell broth against Amylobora (Table 3). Both the cell broth containing live cells of E. 0617-T307 and the suspension containing 2 mg/mL RejuAgro A were derived from E. 0617-T307. It showed antibacterial activity against Amylobora. However, no inhibition circle was observed when applying Serenade®.
0617-T307細胞と活性成分RejuAgro Aの両方からなる生物学的制御方法を見つけるために、以下のような実験が行われた。RejuAgro Aの生産菌である0617-T307に対する抗菌アッセイのために、RejuAgro Aを含む0617-T307の40時間培養した細胞ブロスの上清(「上清」と略記)を使用した。0617-T307菌株はYME培地ではなく、LB培地で上清の2倍希釈で増殖できることが示された。上清の抑制効果は、pH値が低いことに起因することをさらなる研究が示した。次いでpHを6.5~6.8に制御することで、質問1及び2に「はい」と答えることができる。
In order to find a biological control method consisting of both 0617-T307 cells and the active ingredient RejuAgro A, the following experiments were conducted. For the antibacterial assay against 0617-T307, the producer of RejuAgro A, the supernatant (abbreviated as "supernatant") of cell broth cultured for 40 hours of 0617-T307 containing RejuAgro A was used. It was shown that the 0617-T307 strain could be grown in LB medium, but not in YME medium, by diluting the supernatant two-fold. Further studies showed that the inhibitory effect of the supernatant was due to the low pH value. By then controlling the pH to 6.5 to 6.8,
生物活性フラクション(粗抽出物、100μg/mL;flash-RejuAgro A、20μg/mL;HPLC-RejuAgro A、10μg/mL)を菌株0617-T307、Ea及びXacに対して試験した。生物活性フラクションは菌株0617-T307の増殖を抑制することができなかったことが示され、このことは生物的制御剤を調製するために、RejuAgro Aは0617-T307細胞と混合できることを示す。RejuAgro Aを含む生物活性フラクションは、Ea及びXacに対して阻害効果を示し、特にflash-RejuAgro A及びHPLC-RejuAgro Aは、試験条件下でEa及びXacの増殖をほぼ停止させた。このことは、RejuAgro A溶液は、10~20μg/mLで火傷病及び柑橘類がん腫病の生物的制御に使用され得ることを実証する。 The bioactive fraction (crude extract, 100 μg/mL; flash-RejuAgro A, 20 μg/mL; HPLC-RejuAgro A, 10 μg/mL) was tested against strains 0617-T307, Ea and Xac. It was shown that the bioactive fraction was not able to inhibit the growth of strain 0617-T307, indicating that RejuAgro A can be mixed with 0617-T307 cells to prepare a biocontrol agent. The bioactive fraction containing RejuAgro A showed an inhibitory effect on Ea and Xac, especially flash-RejuAgro A and HPLC-RejuAgro A almost stopped the proliferation of Ea and Xac under the tested conditions. This demonstrates that RejuAgro A solution can be used for biocontrol of fire blight and citrus carcinoma disease at 10-20 μg/mL.
[実施例6] 0617-T307菌株の酸性化上清(pH2.0)の酢酸エチル抽出物由来の生物活性代謝物の同定及び特徴付け。 Example 6 Identification and characterization of bioactive metabolites from ethyl acetate extract of acidified supernatant (pH 2.0) of strain 0617-T307.
ストック細菌であるシュードモナス属種0617-T307を、LB寒天(10g/L トリプトン、5g/L 酵母エキス、10g/L NaCl、15g/L 寒天、水)プレートに接種し、28℃インキュベーターで24時間増殖させた。種培地の調製については、0617-T307の単一コロニーを、500mLのオートクレーブしたYME培地(4g/L 酵母エキス、4g/L グルコース、10g/L 麦芽エキス)に接種し、28℃で150rpmの振盪速度で24時間増殖させる。次いで、2LのオートクレーブしたYME培地をそれぞれ含む8つの4Lフラスコに種培地を接種した。16℃、振盪速度150rpmの振盪機で7日間発酵を進行させた。 Stock bacteria Pseudomonas sp. 0617-T307 was inoculated onto LB agar (10 g/L tryptone, 5 g/L yeast extract, 10 g/L NaCl, 15 g/L agar, water) plates and grown in an incubator at 28°C for 24 hours. I let it happen. For seed medium preparation, a single colony of 0617-T307 was inoculated into 500 mL of autoclaved YME medium (4 g/L yeast extract, 4 g/L glucose, 10 g/L malt extract) and shaken at 150 rpm at 28 °C. Grow at speed for 24 hours. The seed medium was then inoculated into eight 4L flasks each containing 2L of autoclaved YME medium. Fermentation proceeded for 7 days in a shaker at 16° C. and a shaking speed of 150 rpm.
7日間の増殖後、上清は、細菌培養物を4000rpmで15分間遠心分離することによって得られた。次いで、上清のpHは、6N HClを加えることによって2.0に調整された。次いで、酸性化した上清は、酢酸エチル抽出に供せられた。この結果、0617-T307菌株の14L培養物から3.0gの粗抽出物が得られた。 After 7 days of growth, the supernatant was obtained by centrifuging the bacterial culture at 4000 rpm for 15 min. The pH of the supernatant was then adjusted to 2.0 by adding 6N HCl. The acidified supernatant was then subjected to ethyl acetate extraction. As a result, 3.0 g of crude extract was obtained from a 14 L culture of strain 0617-T307.
濃縮した試料はアセトンに溶解され、シリカゲルと混合されてUV検出器を備えたフラッシュクロマトグラフィーシステム(Yamazen AI-580)のシリカゲルカラム(φ3.0×20cm)の上に装填された。試料を装填した後、試料は、極性が増加する順に、100%ヘキサン、75%ヘキサン/25%酢酸エチル、50%ヘキサン/50%酢酸エチル、25%ヘキサン/75%酢酸エチル、100%酢酸エチル、50%酢酸エチル/50%アセトン、100%アセトン、及び100%メタノールのそれぞれの溶媒280mLによって溶出された。試料は20mL/分の流速で溶出された。溶出液はUV254nmでモニターされ、フラクションは20mL/試験管の時間モードにより回収された。フラッシュクロマトグラフィーから得られたフラクション又は試験管は合計114本であった。 The concentrated sample was dissolved in acetone, mixed with silica gel, and loaded onto a silica gel column (φ3.0×20 cm) of a flash chromatography system (Yamazen AI-580) equipped with a UV detector. After loading the samples, the samples were tested in order of increasing polarity: 100% hexane, 75% hexane/25% ethyl acetate, 50% hexane/50% ethyl acetate, 25% hexane/75% ethyl acetate, 100% ethyl acetate. , 50% ethyl acetate/50% acetone, 100% acetone, and 100% methanol. Samples were eluted at a flow rate of 20 mL/min. The eluate was monitored by UV 254 nm and fractions were collected by time mode at 20 mL/tube. A total of 114 fractions or test tubes were obtained from flash chromatography.
生成されたフラクションは、その後のプレートアッセイに適用された。それぞれのフラクションの1mLを1.5mL試験管に採取し、エッペンドルフ真空濃縮機で真空乾燥させた。乾燥された試料は、50μLのDMSOに溶解され、そのうちの2μLがプレートアッセイに使用された。簡単に説明すると、エルウィニア・アミロボーラ 273を、50%LB(5.0g/L トリプトン、2.5g/L 酵母エキス、5.0g/L NaCl)プレートに接種し、単一コロニーを5mL LB培地に接種することになる。細菌は滅菌水で1:100に希釈されることになり、そのうちの225μLが50%LBプレートにプレーティングされた。バイオセーフティキャビネット内で10分間乾燥させた後、それぞれのフラクションのDMSO溶液をシャーレのあらかじめラベルを貼った部分に分配し、さらに10分間乾燥させた。アッセイに伴い、DMSO及びカスガマイシンをそれぞれ陰性対照及び陽性対照として使用した。次いで、プレートは28℃のインキュベーターでインキュベートされ、1日後に阻止円が確認される。 The generated fractions were applied to subsequent plate assays. 1 mL of each fraction was collected in a 1.5 mL test tube and vacuum dried in an Eppendorf vacuum concentrator. The dried sample was dissolved in 50 μL of DMSO, of which 2 μL was used for plate assay. Briefly, Erwinia amylovora 273 was inoculated onto 50% LB (5.0 g/L tryptone, 2.5 g/L yeast extract, 5.0 g/L NaCl) plates, and single colonies were transferred to 5 mL LB medium. I will be vaccinated. Bacteria were to be diluted 1:100 in sterile water, of which 225 μL was plated on 50% LB plates. After drying in a biosafety cabinet for 10 minutes, the DMSO solution of each fraction was dispensed onto a pre-labeled area of the Petri dish and allowed to dry for an additional 10 minutes. Along with the assay, DMSO and kasugamycin were used as negative and positive controls, respectively. The plates are then incubated in a 28° C. incubator and inhibition zones are confirmed after one day.
114のフラッシュフラクションのインビトロプレートアッセイでは、E.アミロボーラ273の増殖を抑制する3つの生物活性フラクション(T3234、T5058、T7882)が示された。フラクション3234及び5258は、比較的小さなクリアランスゾーンを示した。フラクション3234は、50%ヘキサン/50%酢酸エチルによって溶出される。フラクション5058は、25%ヘキサン/75%酢酸エチルにより溶出された。陰性対照では、DMSOは阻止円を示さず、陽性対照のカスガマイシンは阻止円を示した。別のフラッシュフラクションT7882は、アセトン/酢酸エチル(50%/50%)によって溶出された。これは、E.アミロボーラ活性の増殖を同様に阻害した。 In an in vitro plate assay of 114 flash fractions, E. Three bioactive fractions (T3234, T5058, T7882) were shown to inhibit the growth of Amylobora 273. Fractions 3234 and 5258 showed relatively small clearance zones. Fraction 3234 is eluted with 50% hexane/50% ethyl acetate. Fraction 5058 was eluted with 25% hexane/75% ethyl acetate. As a negative control, DMSO did not show a circle of inhibition, and a positive control, kasugamycin, showed a circle of inhibition. Another flash fraction, T7882, was eluted with acetone/ethyl acetate (50%/50%). This is E. The proliferation of Amylobora activity was similarly inhibited.
さらに抗E.アミロボーラ活性に基づくHPLCによる単離及び精製は、T5058から2つの抗菌性化合物(Rt22.9及びRt25.0)(化合物の式、0617_T307_5058_Rt22.9及び0617_T307_5058_Rt25.0を参照)、T7882から1つの抗菌性化合物(Rt18.9)(化合物の式0617_T307_7882_Rt18.9を参照)を同定した。T307_5058_Rt22.9及びT307_5058_Rt25.0はトリプトファン由来の天然物であり、その構造はScifinderデータベースで報告されているが生物活性は報告されていない(Lootsら、(2015))。0617_T307_7882_Rt18は、以前に報告されているジフリルの誘導体であると予測された(Osipovら、(1978))。これらの天然物は以下に示されている: Furthermore, anti-E. Isolation and purification by HPLC based on Amylobora activity resulted in two antibacterial compounds (Rt22.9 and Rt25.0) from T5058 (see compound formulas, 0617_T307_5058_Rt22.9 and 0617_T307_5058_Rt25.0), one antibacterial compound from T7882 The compound (Rt18.9) (see compound formula 0617_T307_7882_Rt18.9) was identified. T307_5058_Rt22.9 and T307_5058_Rt25.0 are tryptophan-derived natural products whose structures have been reported in the Scifinder database but no biological activity (Loots et al. (2015)). 0617_T307_7882_Rt18 was predicted to be a previously reported derivative of difuryl (Osipov et al. (1978)). These natural products are shown below:
[実施例7] LCMSMS及びスペクトルライブラリ検索を使用した0617-T307菌株由来のその他の代謝物の同定。 Example 7 Identification of other metabolites from strain 0617-T307 using LCMSMS and spectral library searching.
非pH調整細胞ブロス及びpH調整細胞ブロス(6N HClにより細胞ブロスのpHは2.0に調整された)の粗抽出物は濃縮され、内部標準(m/z311.08)を含む250μL 100% MeOHに再懸濁され、LC-MS/MS分析に使用された。LC注入量:5μL;LCカラム:1.7μM C18、100A、Phenomenexからの50×2.1mm Kinetex C18カラム、12分のグラジエント。Bruker Maxis Impact IIで5~95% ACN。データは、Bruker MaXis Impact II、UHR-QqTOF(超高分解能Qq-Time-Of-Flight)質量分析装置によって取得した。各フルMSスキャンに続いて、スペクトル中の最も豊富な8つのイオンの衝突活性化解離法(CID)フラグメンテーションを用いたタンデムMS(MS/MS)を実施した。スキャン速度は3Hzであった。 Crude extracts of non-pH adjusted cell broth and pH adjusted cell broth (pH of cell broth was adjusted to 2.0 with 6N HCl) were concentrated and added to 250 μL 100% MeOH containing internal standard (m/z 311.08). and used for LC-MS/MS analysis. LC injection volume: 5 μL; LC column: 1.7 μM C18, 100A, 50 x 2.1 mm Kinetex C18 column from Phenomenex, 12 min gradient. 5-95% ACN with Bruker Maxis Impact II. Data were acquired by a Bruker MaXis Impact II, UHR-QqTOF (Ultra High Resolution Qq-Time-Of-Flight) mass spectrometer. Each full MS scan was followed by tandem MS (MS/MS) using collisionally activated dissociation (CID) fragmentation of the eight most abundant ions in the spectrum. The scan rate was 3Hz.
次いで、バイオインフォマティクス解析及び分子ネットワーク解析に基づき、新規化合物及び既知化合物の同定を目的として、正確なスペクトルライブラリ検索が実施された。試料のMS/MSスペクトルは、以下のスペクトルライブラリに対して検索された、1)GNPS Community Library、2)FDA Library、PhytoChemical Library、3)NIH Clinical Collections、4)NIH Natural Products Library、5)Pharamacologically Active NIH Small Molecule Repository、6)Faulkner Legacy Library、7)Pesticides、8)Dereplicator Identified MS/MS Peptidic Natural Products、9)PNNL Lipids、10)Massbank、11)Massbank EU、12)MoNA、13)ReSpect-Phytochemicals、14)HMDB。 A precise spectral library search was then performed based on bioinformatics analysis and molecular network analysis with the aim of identifying new and known compounds. The MS/MS spectra of the samples were searched against the following spectral libraries: 1) GNPS Community Library, 2) FDA Library, PhytoChemical Library, 3) NIH Clinical Collections, 4) NIH Natural Pr 5) Pharmacologically Active NIH Small Molecule Repository, 6) Faulkner Legacy Library, 7) Pesticides, 8) Dereplicator Identified MS/MS Peptidic Natural Produ cts, 9) PNNL Lipids, 10) Massbank, 11) Massbank EU, 12) MoNA, 13) ReSpect-Phytochemicals, 14) HMDB.
試料のMS/MSスペクトルは上記のライブラリで検索され、参照スペクトルにオフセットして整列させた。マッチングパラメーターは同じであった。これらの結果は、既知化合物の構造類似体を同定するために探索され得る。MS/MS分子ネットワークは、最小クラスタサイズ=2、最小エッジ0.7コサイン、最小マッチングピーク数6で生成された。例として、m/z303.16の新しい分子種は、活性フラクション0617-T307_5058_Rt25.0からの新しい化合物に対応するものであることが同定された。粗抽出物から既知化合物の一部が確認され、粗抽出物は植物成長促進因子であるインドール-3-カルボン酸及びキサントリジン(xantholysin)Aを含む。1)P.プチダ BW11M1の幅広い抗真菌活性は主にキサントリジン生産に依存する、2)キサントリシンはスウォーミングに必要でバイオフィルム形成に寄与している、と報告されている(Liら、(2013))。実際に、0617-T307、0418-T328、及び0318-T327を28℃で培養することにより、より高い濃度のキサントリジンAが観察された。つまり、生物活性化合物であるRejuAgro Aを除けば、キサントリジンAは生物的制御細菌0617-T307とその近縁種0318-T3027及び0418-T328の抗菌活性に寄与する代謝物である。 The MS/MS spectra of the samples were searched in the library described above and aligned with an offset to the reference spectrum. Matching parameters were the same. These results can be explored to identify structural analogs of known compounds. MS/MS molecular networks were generated with minimum cluster size = 2, minimum edge 0.7 cosine, and minimum number of matching peaks 6. As an example, a new molecular species with m/z 303.16 was identified that corresponds to a new compound from active fraction 0617-T307_5058_Rt25.0. Some of the known compounds were confirmed from the crude extract, and the crude extract contains indole-3-carboxylic acid and xantholysin A, which are plant growth promoting factors. 1) P. It has been reported that the broad antifungal activity of P. putida BW11M1 mainly depends on xantholysine production; 2) xantholysine is required for swarming and contributes to biofilm formation (Li et al. (2013)). In fact, higher concentrations of xantholysine A were observed by culturing 0617-T307, 0418-T328, and 0318-T327 at 28°C. That is, except for the bioactive compound RejuAgro A, xantholysine A is a metabolite that contributes to the antibacterial activity of the biocontrol bacteria 0617-T307 and its relatives 0318-T3027 and 0418-T328.
[実施例8] RejuAgro Aを生産する菌株0617-T307及びそのいくつかの近縁種の温室及び野外感染アッセイ。 Example 8 Greenhouse and field infection assays of RejuAgro A producing strain 0617-T307 and several of its relatives.
エルウィニア・アミロボーラに対する0617-T307の生物制御活性を評価するため、University of Wisconsin-Milwaukeeの温室でクラブアップルの木を用いた感染アッセイを行った。1.0×108cfu/mLを含む生物制御剤(0617-T307、0717-T327、0617-T318)は、複数本の小区画にある花(80%~満開)に散布された。簡単に説明すると、菌株0617-T307を5mLのLB培地を含む26mLガラス管で一晩増殖させ、次いでその細胞をLB培地に接種(1:100)して28℃、200rpmの振盪機で14~18時間増殖させた。細胞が採取され、108CFU/mLとなるまで10倍の水に再懸濁させた。この再懸濁液は、温室及び野外での火傷病制御のための野外アッセイに使用され得る。対照花には蒸留水が散布された。次いで、すべての花に、1.0×106cfu/mLのE.アミロボーラ菌株エルウィニア・アミロボーラ 273を散布することによって接種した。0617-T307による処理は、2018年9月7日、10月9日、及び10月19日に3回実施した。表4を参照すると、0617-T307(シュードモナス・ソリ)のすべての散布処理は、クラブアップルの花に蒸留水の0%制御に対して花枯病症状の100%制御をもたらし、0617-T307がE.アミロボーラによる火傷病に対する有望な生物制御剤となることが示唆された。他の2つのシュードモナス属種、0717-T327(シュードモナス・コーリエンシス)及び0617-T318(シュードモナス・プロテゲンス)の制御率はそれぞれ16.7%と25%と低かった。結論として,今回試験した3種のシュードモナス属種のうち、0617-T307のみがクラブアップルの火傷病に対して良好な制御効果を示す。植物毒性は認められなかった。 To evaluate the biocontrol activity of 0617-T307 against Erwinia amylovora, infection assays were performed using crabapple trees in a greenhouse at the University of Wisconsin-Milwaukee. Biocontrol agents (0617-T307, 0717-T327, 0617-T318) containing 1.0×10 8 cfu/mL were applied to flowers (80% to full bloom) in multiple plots. Briefly, strain 0617-T307 was grown overnight in a 26 mL glass tube containing 5 mL of LB medium, then the cells were inoculated (1:100) into LB medium and incubated at 28°C on a shaker at 200 rpm for 14 to 30 minutes. Grow for 18 hours. Cells were harvested and resuspended in 10x water to 10 8 CFU/mL. This resuspension can be used in field assays for fire blight control in greenhouses and fields. Control flowers were sprayed with distilled water. All flowers were then injected with 1.0 x 10 6 cfu/mL of E. It was inoculated by spraying the Amylovora strain Erwinia amylovora 273. The treatment using 0617-T307 was carried out three times on September 7, October 9, and October 19, 2018. Referring to Table 4, all spray treatments of 0617-T307 (Pseudomonas sori) resulted in 100% control of flower blight symptoms against 0% control of distilled water on crabapple flowers; E. It was suggested that it could be a promising biological control agent for fire blight caused by Amylobora. Control rates for the other two Pseudomonas species, 0717-T327 (Pseudomonas coriensis) and 0617-T318 (Pseudomonas protegens), were lower at 16.7% and 25%, respectively. In conclusion, among the three Pseudomonas species tested, only 0617-T307 shows a good control effect on crabapple fire blight. No phytotoxicity was observed.
野外アッセイでは、2019年5月5日及び5月6日(リンゴの花の40%及び70%開花)に、RejuAgro Aを生産する生物的制御細菌(0617-T307、0118-T319、0318-T327、0418-T328;表2参照)は5×108CFU/mLの濃度で果樹園内のリンゴ木の花に適用された。細菌性病原菌E.アミロボーラ Ea110は、5月7日(90%開花)に、5×106CFU/mLの濃度で接種された。水対照、ストレプトマイシン、0617-T307、0118-T319、0318-T327、及び0418-T328の罹病花房率はそれぞれ32.9%、13.3%、16.8%、18.5%、16.7%、11.8%である。ストレプトマイシンと比較して、RejuAgro Aを生産する生物的制御細菌は、リンゴ園の火傷病の制御に対して同等かそれ以上の効果を有する。 In field assays, biocontrol bacteria producing RejuAgro A (0617-T307, 0118-T319, 0318-T327 , 0418-T328; see Table 2) was applied to the flowers of apple trees in an orchard at a concentration of 5×10 8 CFU/mL. Bacterial pathogen E. Amylobora Ea110 was inoculated on May 7th (90% flowering) at a concentration of 5×10 6 CFU/mL. The diseased inflorescence rates for water control, streptomycin, 0617-T307, 0118-T319, 0318-T327, and 0418-T328 were 32.9%, 13.3%, 16.8%, 18.5%, and 16.7, respectively. %, 11.8%. Compared to streptomycin, the biocontrol bacteria producing RejuAgro A is equally or more effective in controlling fire blight in apple orchards.
[実施例9] RejuAgro A及びBとその生産菌のベンチュリア・イナエキュアリスに対する抗真菌活性。 [Example 9] Antifungal activity of RejuAgro A and B and their producing bacteria against Venturia inaequalis.
リンゴ赤かび病を引き起こす真菌ベンチュリア・イナエキュアリスをPDA寒天培地で暗所、室温(約24℃)で維持した。PDA(ポテトデキストロースアガー)から、分生子及び菌糸の混合懸濁液(0.01M PBS中)が採取された。10μLの分生子及び菌糸の懸濁液を、生物的制御細菌、RejuAgro A、又はRejuAgro A改良プレートに滴下した。対照は、生物的制御細菌、RejuAgro A又はBを添加しないPDAプレートであった。シャーレは、暗所の室温でインキュベートされ、7日後にV.イナエキュアリスのそれぞれのコロニーの直径が確認された。 The fungus Venturia inaequalis, which causes apple head blight, was maintained on PDA agar in the dark at room temperature (approximately 24°C). A mixed suspension of conidia and mycelia (in 0.01 M PBS) was collected from PDA (potato dextrose agar). 10 μL of conidial and hyphal suspensions were dropped onto biological control bacteria, RejuAgro A, or RejuAgro A modified plates. Controls were PDA plates without the addition of biocontrol bacteria, RejuAgro A or B. Petri dishes were incubated at room temperature in the dark and after 7 days V. The diameter of each colony of Ina equalis was confirmed.
対照(図4)と比較した場合、選択された4つの生物的制御細菌株0617-T307、0118-T319、0318-T327、及び0418-T328は、PDAプレート上のV.イナエキュアリスの増殖を抑制することができる(図5)。RejuAgro Aは、40~80μg/mLでPDAプレート上のV.イナエキュアリスの増殖を抑制できる(図6)。しかし、10~80μg/mLでPDAプレート上において、V.イナエキュアリスの増殖に対するRejuAgro Bの抑制作用は観察されなかった(図7)。最後に、200~1000μg/mLの硫酸銅を含むPDAプレート上において、V.イナエキュアリスの抑制は観察されなかった(図8)。 When compared to the control (Figure 4), the four selected biocontrol bacterial strains 0617-T307, 0118-T319, 0318-T327, and 0418-T328 were found to be more susceptible to V. The proliferation of Ina equalis can be suppressed (Fig. 5). RejuAgro A was added to V.I. on PDA plates at 40-80 μg/mL. The proliferation of Ina equalis can be suppressed (Figure 6). However, on PDA plates at 10-80 μg/mL, V. No inhibitory effect of RejuAgro B on the proliferation of Ina equalis was observed (FIG. 7). Finally, V. No inhibition of Ina equalis was observed (Figure 8).
[実施例10] シュードモナス属種によるRejuAgro Aの生産 [Example 10] Production of RejuAgro A by Pseudomonas sp.
RejuAgro Aの量は、500mLのYME培地を含む4Lフラスコを16℃、220rpmの振盪条件で24時間発酵させた後のブロスについて、HPLC-MSによって分析された。HPLCピーク面積とRejuAgro Aの量との関係を調べるために、量-ピーク面積曲線が作成された(図9)。分析方法:1)25mLの細胞ブロスは25mLの酢酸エチルで抽出された。2)5mLの酢酸エチル抽出物は乾燥され、0.1mLのメタノールに溶解された。3)4μLがHPLC-MSに注入された。 The amount of RejuAgro A was analyzed by HPLC-MS in the broth after 24 hours of fermentation in a 4L flask containing 500 mL of YME medium at 16° C. and shaking at 220 rpm. To investigate the relationship between HPLC peak area and amount of RejuAgro A, an amount-peak area curve was constructed (Figure 9). Analytical method: 1) 25 mL of cell broth was extracted with 25 mL of ethyl acetate. 2) 5 mL of ethyl acetate extract was dried and dissolved in 0.1 mL of methanol. 3) 4 μL was injected into HPLC-MS.
7種類の細菌(0617-T307、0917-T305、0917-T306、0917-T307、0118-T319、0318-T327、0418-T328)がRejuAgro Aの生産について評価され、種培地は、細菌をYME培地で16℃、220rpmで24時間増殖させることによって調製された。HPLC分析は、7種類の細菌すべてがRejuAgro Aを生産することを示した(図10)。 Seven types of bacteria (0617-T307, 0917-T305, 0917-T306, 0917-T307, 0118-T319, 0318-T327, 0418-T328) were evaluated for the production of RejuAgro A, and the seed medium was were prepared by growing for 24 hours at 16°C and 220 rpm. HPLC analysis showed that all seven bacteria produced RejuAgro A (Figure 10).
[実施例11] RejuAgro Aの製剤化及び温室アッセイ。 Example 11 RejuAgro A formulation and greenhouse assay.
RejuAgro Aの製剤化(溶液、SL;表5参照)。花に適用する前に、10μg/mLが毒性緩和剤として1%のポリエチレングリコール(PEG)4000とタンク混合された。その後の試験で、毒性緩和剤として0.03%のポリビニルアルコール(PVA)を使用すると、より優れた花の保護効果が得られることが示された。また、界面活性物質であるAlligare90は、より高い効果を得るために添加することができる(表6)。 Formulation of RejuAgro A (solution, SL; see Table 5). Prior to application to flowers, 10 μg/mL was tank mixed with 1% polyethylene glycol (PEG) 4000 as a safener. Subsequent tests showed that using 0.03% polyvinyl alcohol (PVA) as a safener provided better flower protection. Additionally, Alligare 90, a surfactant, can be added to obtain a higher effect (Table 6).
エルウィニア・アミロボーラに対するRejuAgro Aの生物制御活性を評価するため、University of Wisconsin-Milwaukeeにおいて、クラブアップルの木を用いた温室感染アッセイが実施された。10μg/mLに1%ポリエチレングリコール(PEG)4000を添加したもの又は1%PEG4000(陰性対照)を、接種3時間前と接種24時間後に満開の木花に適用した。接種には、水に懸濁したE.アミロボーラ110菌株を約108CFU/mLが使用された。感染率は接種後6日目前後に算出された。実験は2020年1月24日~1月31日の1週間に実施された。RejuAgro Aは、花枯病を効果的に抑制することができる(表6)。
To evaluate the biocontrol activity of RejuAgro A against Erwinia amylovora, a greenhouse infection assay using crabapple trees was conducted at the University of Wisconsin-Milwaukee. 10 μg/mL with 1% polyethylene glycol (PEG) 4000 or 1% PEG 4000 (negative control) was applied to fully bloomed
[実施例12] ボトリティス・シネレア CA17に対する0617-T307細胞ブロスの抗真菌活性 [Example 12] Antifungal activity of 0617-T307 cell broth against Botrytis cinerea CA17
菌株0617-T307の種菌は、YME培地で28℃、180rpmで24時間増殖させることにより調製された。次いで、4%(2mL~50mL)を50mLのM8(IAA培地)又はM9(CN培地)又はM7(PRN培地)又はM6(DAPG培地)を含む250mLフラスコに接種し、28℃、180rpmで48時間増殖させた。0.5mLの細胞ブロスが12時間及び24時間に採取され、-20℃のフリーザーで保管された。抗真菌アッセイのために、細胞ブロスが解凍され、PDA(ポテトデキストロースアガー)プレートの試料ウェル上に、ボトリティス・シネレアを接種した中心から半径方向に等しい距離で5μL塗布された(図11)。細胞ブロスは、PDA(ポテトデキストロースアガー)プレート上のボトリティス・シネレア CA17に対して抗真菌活性を有することが示された。 An inoculum of strain 0617-T307 was prepared by growing in YME medium at 28°C and 180 rpm for 24 hours. Then, 4% (2 mL to 50 mL) was inoculated into a 250 mL flask containing 50 mL of M8 (IAA medium) or M9 (CN medium) or M7 (PRN medium) or M6 (DAPG medium) and incubated at 28° C. and 180 rpm for 48 hours. Proliferated. 0.5 mL of cell broth was harvested at 12 and 24 hours and stored in a -20°C freezer. For antifungal assays, cell broth was thawed and 5 μL spread onto sample wells of PDA (potato dextrose agar) plates at equal radial distances from the center of the Botrytis cinerea inoculation (Figure 11). Cell broth was shown to have antifungal activity against Botrytis cinerea CA17 on PDA (potato dextrose agar) plates.
[実施例13] 粗抽出物、RejuAgro A及びRejuAgro Bの植物病原性細菌に対する抗菌活性。 [Example 13] Antibacterial activity of crude extracts, RejuAgro A and RejuAgro B against phytopathogenic bacteria.
細菌0917-T305、0318-T327及び0418-T328の代謝物は、R.ソラナセアラム、C.ミシガンエンシス 亜種ミシガンエンシス及びX.アルボリコーラ 病原型ジュグランディスに対して優れた効果を示した(表7)。細菌0917-T305、0318-T327及び0418-T328は、YME培地でそれぞれ16℃及び28℃で増殖させた。0917-T305、0318-T327及び0418-T328の天然物抽出物は5mg/mLで調製され、それらを3種類の植物病原菌、ラルストニア・ソラナセアラム、クラビバクター・ミシガンエンシス 亜種ミシガンエンシス、及びキサントモナス・アルボリコーラ 病原型ジュグランディスに対してプレート拡散アッセイにより試験された。寒天プレート拡散アッセイでは、16℃と28℃のYMEで増殖させた細菌0917-T305、0318-T327、0418-T328の代謝物が、試験したR.ソラナセアラム、C.ミシガンエンシス 亜種ミシガンエンシス、X.アルボリコーラ 病原型ジュグランディスに対して比較的良い効果を示した(表7)。このことは、RejuAgro Aとともに、他の代謝物もラルストニア・ソラナセアラム、クラビバクター・ミシガンエンシス 亜種ミシガンエンシス、キサントモナス・アルボリコーラ 病原型ジュグランディスに対して優れた効果を有することを示す。RejuAgro Bは、ラルストニア・ソラナセアラムに対して良好な効果を示す(表7)。 The metabolites of bacteria 0917-T305, 0318-T327 and 0418-T328 are R. Solanacearum, C. michiganensis subspecies michiganensis and X. michiganensis. It showed excellent efficacy against Arboricola arboricola pathogenic type Jugrandis (Table 7). Bacteria 0917-T305, 0318-T327 and 0418-T328 were grown in YME medium at 16°C and 28°C, respectively. Natural product extracts of 0917-T305, 0318-T327 and 0418-T328 were prepared at 5 mg/mL and combined with three plant pathogens, Ralstonia solanacearum, Clavibacter michiganensis subsp. michiganensis, and Xanthomonas arboricola. It was tested by plate diffusion assay against the pathogenic type S. jugrandis. In agar plate diffusion assays, metabolites of bacteria 0917-T305, 0318-T327, 0418-T328 grown in YME at 16°C and 28°C were compared to the tested R. Solanacearum, C. michiganensis subspecies michiganensis, X. It showed a relatively good effect against Arboricola pathotype Jugrandis (Table 7). This indicates that, along with RejuAgro A, other metabolites also have excellent effects against Ralstonia solanacearum, Clavibacter michiganiensis subspecies michiganensis, and Xanthomonas arboricola pathotype juglandis. RejuAgro B shows good efficacy against Ralstonia solanacearum (Table 7).
[実施例14] Rt18.9、Rt22.9、及びRt25.0の抗菌効果。 [Example 14] Antibacterial effects of Rt18.9, Rt22.9, and Rt25.0.
ストック細菌であるシュードモナス属種0617-T307は、LB寒天(10g/L トリプトン、5g/L 酵母エキス、10g/L NaCl、15g/L 寒天、水)プレートに接種され、28℃インキュベーターで24時間増殖させた。発酵及び粗抽出物の調製は実施例6に記載されたものと同様に実施された。 Stock bacteria Pseudomonas sp. 0617-T307 were inoculated onto LB agar (10 g/L tryptone, 5 g/L yeast extract, 10 g/L NaCl, 15 g/L agar, water) plates and grown for 24 hours in a 28°C incubator. I let it happen. Fermentation and crude extract preparation were carried out similarly to that described in Example 6.
シュードモナス属種0617-T307の酸性化細胞ブロスの酢酸エチル抽出物のHPLCによる分離及び精製は、フラッシュフラクションT5058から2種類の抗菌性化合物(Rt22.9及びRt25.0)、フラッシュフラクションT7882から1種類の抗菌性化合物(Rt18.9)を同定した。これらは、表8に示された細菌株に対して抗菌活性について試験された。DMSO、Rt18.9、Rt22.9又はRt25.0の2μLが、異なる細菌株が増殖した寒天プレートにそれぞれスポットされ、阻止円がさらに試験された(表8)。 HPLC separation and purification of ethyl acetate extract of acidified cell broth of Pseudomonas sp. antibacterial compound (Rt18.9) was identified. These were tested for antibacterial activity against the bacterial strains shown in Table 8. 2 μL of DMSO, Rt18.9, Rt22.9 or Rt25.0 were each spotted on agar plates on which different bacterial strains were grown and the inhibition zones were further tested (Table 8).
[実施例15] ミコスフェレラ・フィジエンシスに対するRejuAgro Aの抗菌効果 [Example 15] Antibacterial effect of RejuAgro A against Mycospherella fisiensis
ミコスフェレラ・フィジエンシスに対するRejuAgro Aの抗菌効果は、HPLCで精製したRejuAgro Aの最終濃度60μg/mLと600μg/mLをそれぞれPDA寒天培地に添加することによって検討された。0.5mg/mL又は5mg/mL RejuAgro Aの480μLは、6ウェルプレートのウェル内の3.52mLのPDAに添加され、RejuAgro Aの最終濃度がそれぞれ60μg/mL(図12、中央のウェル(パネルA))及び600μg/mL(図12、左のウェル(パネルB))になるようにした。プレートは穏やかに振盪され、化合物を溶解させた。3.52mLのPDAを含む480μLの水が対照処理として使用された(図12、右のウェル(パネルC))。寒天の固化後、M.フィジエンシスを増殖させた寒天片が寒天表面の中央に配置された。M.フィジエンシスの増殖の完全な抑制は、RejuAgro Aの600μg/mLの濃度で処理した場合、接種後2週間に確認された(図12)。 The antibacterial effect of RejuAgro A against Mycosphaerella fisiensis was examined by adding final concentrations of HPLC-purified RejuAgro A of 60 μg/mL and 600 μg/mL to PDA agar medium, respectively. 480 μL of 0.5 mg/mL or 5 mg/mL RejuAgro A was added to 3.52 mL of PDA in the wells of a 6-well plate, resulting in a final concentration of RejuAgro A of 60 μg/mL each (Figure 12, center well (panel). A)) and 600 μg/mL (Figure 12, left well (panel B)). The plate was gently shaken to dissolve the compound. 480 μL of water containing 3.52 mL of PDA was used as a control treatment (Figure 12, right well (panel C)). After solidification of the agar, M. A piece of agar on which P. fisiensis was grown was placed in the center of the agar surface. M. A complete inhibition of the growth of S. physiensis was confirmed 2 weeks after inoculation when treated with RejuAgro A at a concentration of 600 μg/mL (FIG. 12).
[実施例16] キサントモナス・オリザエ 病原型オリザエ(Xon507)に対するRejuAgro Aの抗菌効果 [Example 16] Antibacterial effect of RejuAgro A against Xanthomonas oryzae pathogenic type oryzae (Xon507)
キサントモナス・オリザエ 病原型オリザエ(Xon507)に対するRejuAgro Aの抗菌効果が検討された。X.オリザエ 病原型オリザエ(Xon507)の細菌懸濁液(OD600=0.3)がPSG寒天プレートに噴霧された。HPLCにより精製された水性RejuAgro Aをそれぞれ5.5μg/mL、11.1μg/mL、22.1μg/mL、33.2μg/mL、55.4μg/mL、110.7μg/mLの濃度で50μLの装填体積で装填したペーパーディスクは寒天プレートに配置され、ペーパーディスクを置いて44時間後に阻止円が計測された。阻害は、RejuAgro A懸濁液を染み込ませたペーパーディスクのすべての濃度で観察された(表9)。 The antibacterial effect of RejuAgro A against Xanthomonas oryzae (Xon507) was investigated. X. A bacterial suspension ( OD600 = 0.3) of S. oryzae (Xon507) was sprayed onto PSG agar plates. Aqueous RejuAgro A purified by HPLC was added to 50 μL at concentrations of 5.5 μg/mL, 11.1 μg/mL, 22.1 μg/mL, 33.2 μg/mL, 55.4 μg/mL, and 110.7 μg/mL, respectively. Paper disks loaded with the loading volume were placed on agar plates and the inhibition circle was measured 44 hours after placing the paper disks. Inhibition was observed at all concentrations of paper discs impregnated with RejuAgro A suspension (Table 9).
[実施例17] キサントモナス・シトリ 病原型シトリ シトランジェ(Xanthomonas citri pv. citri citrange)(XW19)に対するRejuAgro Aの抗菌効果 [Example 17] Antibacterial effect of RejuAgro A against Xanthomonas citri pv. citri citrange (XW19)
キサントモナス・シトリ 病原型シトリ シトランジェ(XW19)に対するRejuAgro Aの抗菌効果が検討された。X.シトリ 病原型シトリ シトランジェ(XW19)の細菌懸濁液(OD600=0.3)がPSG寒天プレートに噴霧された。HPLCにより精製された水性RejuAgro Aをそれぞれ5.5μg/mL、11.1μg/mL、22.1μg/mL、33.2μg/mL、55.4μg/mL、110.7μg/mLの濃度で50μLの装填体積で装填したペーパーディスクは寒天プレートに配置され、ペーパーディスクを寒天プレートに置いて44時間後に阻止円が計測された。阻害は、RejuAgro Aの濃度が55.37μg/mL及び110.74μg/mLで観察された(表10)。 The antibacterial effect of RejuAgro A against Xanthomonas citri pathogenic type Citri citrangae (XW19) was investigated. X. A bacterial suspension (OD 600 =0.3) of the pathotype Citri citrangea (XW19) was sprayed onto PSG agar plates. Aqueous RejuAgro A purified by HPLC was added to 50 μL at concentrations of 5.5 μg/mL, 11.1 μg/mL, 22.1 μg/mL, 33.2 μg/mL, 55.4 μg/mL, and 110.7 μg/mL, respectively. Paper disks loaded with the loading volume were placed on agar plates, and the inhibition circle was measured 44 hours after placing the paper disks on the agar plates. Inhibition was observed at concentrations of RejuAgro A of 55.37 μg/mL and 110.74 μg/mL (Table 10).
[実施例18] 実施例に使用された培地培養組成 [Example 18] Medium culture composition used in the example
表11は、実施例に使用された例示的な培地組成を含む。 Table 11 includes exemplary media compositions used in the examples.
[実施例19] 細菌株、天然物、及びこれらに引用された文献。 [Example 19] Bacterial strains, natural products, and literature cited therein.
本願に記載され、添付の特許請求の範囲に示された細菌株及び天然物は、微生物学の文献でよく知られたものである。これらの文献は、本明細書に開示された引用された細菌株及び天然物のそれぞれについて、以下の表12に示されており、その内容は参照によりその全体が本明細書に組み込まれる。 The bacterial strains and natural products described in this application and set forth in the appended claims are well known in the microbiological literature. These documents are shown in Table 12 below for each of the cited bacterial strains and natural products disclosed herein, the contents of which are incorporated herein by reference in their entirety.
[実施例20] RejuAgro A、RejuAgro B、及びRejuAgro Cの結晶構造情報。 [Example 20] Crystal structure information of RejuAgro A, RejuAgro B, and RejuAgro C.
A.RejuAgro Aの結晶構造情報
RejuAgro A(C7H7NO3S)の単結晶は、RejuAgro Aのクロロホルム溶液をゆっくり蒸発させることによって得られた。オレンジ色の板状小片が得られた。適当な結晶が選択され、SuperNova、Dua、Cu ホーム/近傍、Atlas回折計に装着された。データ収集中、結晶は100.05(10)Kに保たれた。Olex2(Dolomanovら、(2009))を用いて、構造は直接法(Sheldrick(2008))を用いたShelXS構造解決プログラムによって解かれ、最小二乗法による最小化を用いたShelXL精密化パッケージ(Sheldrick,G.M.(2015))によって精密化された。
A. Crystal structure information of RejuAgro A A single crystal of RejuAgro A (C 7 H 7 NO 3 S) was obtained by slowly evaporating a chloroform solution of RejuAgro A. Orange plate-like pieces were obtained. A suitable crystal was selected and mounted on a SuperNova, Dua, Cu home/nearby, Atlas diffractometer. The crystal was held at 100.05 (10) K during data collection. Using Olex2 (Dolomanov et al. (2009)), structures were solved by the ShelXS structure solver using direct methods (Sheldrick, 2008) and with the ShelXL refinement package (Sheldrick, 2009) using least squares minimization. G.M. (2015)).
データセットは、Cu(Kα)放射線を用いたOxford SuperNova回折計で100Kで収集された。 Data sets were collected at 100K on an Oxford SuperNova diffractometer using Cu (Kα) radiation.
RejuAgro A(C7H7NO3S)(M=185.20g/モル)の結晶データ:単斜晶、空間群P21/n(14番)、a=5.30391(6)Å、b=13.97822(13)Å、c=10.74471(13)Å、β=101.5883(12)°、V=780.367(15)Å3、Z=4、T=100.05(10)K、μ(CuKα)=3.429mm-1、Dcalc=1.576g/cm3、13936反射を測定(10.522°≦2Θ≦140.8°)、1496独立(Rint=0.0220、Rsigma=0.0083)これらはすべての計算で使用された。最終のR1は0.0253(I>2σ(I))、wR2は0.0702(全データ)であった。 Crystal data of RejuAgro A (C 7 H 7 NO 3 S) (M = 185.20 g/mol): monoclinic, space group P2 1 /n (No. 14), a = 5.30391 (6) Å, b = 13.97822 (13) Å, c = 10.74471 (13) Å, β = 101.5883 (12) °, V = 780.367 (15) Å 3 , Z = 4, T = 100.05 ( 10) K, μ(CuKα)=3.429mm −1 , Dcalc=1.576g/cm 3 , 13936 reflections measured (10.522°≦2Θ≦140.8°), 1496 independent (R int =0. 0220, R sigma =0.0083) were used in all calculations. The final R 1 was 0.0253 (I>2σ(I)) and wR 2 was 0.0702 (all data).
精密化モデルの記述は、Olex2で作成され、2018年5月29日にOlexSysのsvn.r3508にコンパイルされた。抑制数-0、拘束数-不明。詳細:1.固定Uiso:1.2倍:全C(H,H,H,H,H,H)基、1.5倍時:全C(H,H,H)基、2.その他:Sof(H6A)=Sof(H6D)=Sof(H6F)=1-FVAR(1);Sof(H6B)=Sof(H6C)=Sof(H6E)=FVAR(1);3.a回転基として精密化した無秩序化Me:C6(H6A,H6B,H6C,H6D,H6E,H6F);b.回転基として精密化した理想化Me:C7(H7A,H7B,H7C)。 The description of the refined model was created in Olex2 and published on May 29, 2018 in OlexSys svn. Compiled to r3508. Number of restraints - 0, number of restraints - unknown. Details: 1. Fixed Uiso: 1.2 times: all C (H, H, H, H, H, H) groups, 1.5 times: all C (H, H, H) groups, 2. Others: Sof(H6A)=Sof(H6D)=Sof(H6F)=1-FVAR(1); Sof(H6B)=Sof(H6C)=Sof(H6E)=FVAR(1);3. a Disordered Me:C6 refined as a rotating group (H6A, H6B, H6C, H6D, H6E, H6F); b. Idealized Me:C7 (H7A, H7B, H7C) refined as a rotating group.
図13Aを参照すると、RejuAgro A分子は、S-Me基が複素環に対して8.7°だけ回転した平面構造を有する。この分子では、C4-C5結合(1.531Å)で顕著なπ共役の切断が見られるが、これは明らかに何らかの軌道上の理由がある。sp2の炭素原子に接続するMe基は、2つの位置で回転的に無秩序である。 Referring to FIG. 13A, the RejuAgro A molecule has a planar structure in which the S-Me group is rotated by 8.7° relative to the heterocycle. This molecule shows significant π-conjugation cleavage at the C4-C5 bond (1.531 Å), which clearly has some orbital reason. The Me group attached to the sp 2 carbon atom is rotationally disordered in two positions.
図13Bを参照すると、結晶中のRejuAgro A分子は、N-H...O相互作用によって、中心対称なH結合二量体を形成する。さらに、これらの二量体は、より弱いC-H...O相互作用を介して[-3 0 1]面に沿って2次元層を形成する。 Referring to FIG. 13B, RejuAgro A molecules in the crystal are NH. .. .. The O interaction forms a centrosymmetric H-bonded dimer. Furthermore, these dimers have a weaker C-H. .. .. A two-dimensional layer is formed along the [-3 0 1] plane through O interaction.
RejuAgro Aの化学構造は以下に示される: The chemical structure of RejuAgro A is shown below:
RejuAgro A分子の追加の結晶学的データは、表13~21に示される。 Additional crystallographic data for RejuAgro A molecules are shown in Tables 13-21.
B.RejuAgro Bの結晶構造情報
RejuAgro B(C12H8N2O6)の単結晶は、RejuAgro Bのメタノール溶液をゆっくり蒸発させることによって得られた。オレンジ色の角錐が得られた。適当な結晶が選択され、SuperNova、Dual、Cu ホーム/近傍、Atlas回折計に装着された。データ収集中、結晶は100.05(10)Kに保たれた。Olex2(Dolomanovら、(2009))を用いて、構造は直接法(Sheldrick(2008))を用いたShelXS構造解決プログラムによって解かれ、最小二乗法による最小化を用いたShelXL精密化パッケージ(Sheldrick(2015))によって精密化された。
B. Crystal structure information of RejuAgro B A single crystal of RejuAgro B (C 12 H 8 N 2 O 6 ) was obtained by slowly evaporating a methanol solution of RejuAgro B. Orange pyramids were obtained. A suitable crystal was selected and mounted on a SuperNova, Dual, Cu home/nearby, Atlas diffractometer. The crystal was held at 100.05 (10) K during data collection. Using Olex2 (Dolomanov et al. (2009)), structures were solved by the ShelXS structure solver using direct methods (Sheldrick (2008)) and with the ShelXL refinement package (Sheldrick (2008)) using least squares minimization. (2015)).
データセットは、Cu(Kα)放射線を用いたOxford SuperNova回折計で100Kで収集された。 Data sets were collected at 100K on an Oxford SuperNova diffractometer using Cu (Kα) radiation.
RejuAgro B(C12H8N2O6)(M=276.20g/モル)の結晶データ:三斜晶、空間群P-1(2番)、a=7.0528(3)Å、b=11.7911(5)Å、c=14.6888(6)Å、α=72.249(4)°、β=79.265(3)°、γ=86.633(3)°、V=1143.02(8)Å3、Z=4、T=100.05(10)K、μ(CuKα)=1.139mm-1、Dcalc=1.605g/cm3、15292反射を測定(7.872°≦2Θ≦141.144°)、4304独立(Rint=0.0258、Rsigma=0.0234)これらはすべての計算で使用された。最終のR1は0.0419(I>2σ(I))、wR2は0.1124(全データ)であった。 Crystal data of RejuAgro B (C 12 H 8 N 2 O 6 ) (M=276.20 g/mol): triclinic, space group P-1 (no. 2), a=7.0528(3) Å, b = 11.7911 (5) Å, c = 14.6888 (6) Å, α = 72.249 (4) °, β = 79.265 (3) °, γ = 86.633 (3) °, V = 1143.02 (8) Å 3 , Z = 4, T = 100.05 (10) K, μ (CuKα) = 1.139 mm -1 , Dcalc = 1.605 g/cm 3 , 15292 reflections measured (7 .872°≦2Θ≦141.144°), 4304 independent (R int =0.0258, R sigma =0.0234), which were used in all calculations. The final R 1 was 0.0419 (I>2σ(I)) and wR 2 was 0.1124 (all data).
精密化モデルの記述は、Olex2で作成され、2018年5月29日にOlexSysのsvn.r3508にコンパイルされた。抑制数-0、拘束数-不明。詳細は以下の通りである。1.固定Uiso:1.2倍:全N(H)基、1.5倍:全C(H,H,H)基、2.a騎乗座標で精密化された芳香族/アミドH:N1(H1),N2(H2),N1A(H1A),N2A(H2A);2.b.回転基として精密化した理想化Me:C6(H6A,H6B,H6C),C12(H12A,H12B,H12C),C6A(H6AC,H6AA,H6AB),C12A(H12D,H12E,H12F)。 The description of the refined model was created in Olex2 and published on May 29, 2018 in OlexSys svn. Compiled to r3508. Number of restraints - 0, number of restraints - unknown. Details are as follows. 1. Fixed Uiso: 1.2 times: all N (H) groups, 1.5 times: all C (H, H, H) groups, 2. Aromatic/amide H refined in a riding coordinates: N1 (H1), N2 (H2), N1A (H1A), N2A (H2A); 2. b. Idealized Me refined as a rotating group: C6 (H6A, H6B, H6C), C12 (H12A, H12B, H12C), C6A (H6AC, H6AA, H6AB), C12A (H12D, H12E, H12F).
図14Aを参照すると、RejuAgro B結晶は、対称的に独立した2つのRejuAgro B分子を含む。それぞれの分子はねじれた構造をしており、連結した複素環の平均面間の二面角は70.3°及び80.6°である。それぞれのヘテロ環には、隣接する2つのカルボニル基間のC(sp2)-C(sp2)結合で顕著なπ共役の切断が見られるが(結合長は1.534~1.539Åの範囲)、これは明らかに何らかの軌道上の理由がある。 Referring to FIG. 14A, a RejuAgro B crystal contains two symmetrically independent RejuAgro B molecules. Each molecule has a twisted structure, and the dihedral angles between the average planes of the connected heterocycles are 70.3° and 80.6°. In each heterocycle, significant π-conjugation cleavage is observed at the C(sp 2 )-C(sp 2 ) bond between two adjacent carbonyl groups (bond length is 1.534-1.539 Å). range), there is clearly some orbital reason for this.
図14Bを参照すると、結晶中のRejuAgro B分子は、N-H...O相互作用によって、中心対称なH結合二量体を形成する。これらの二量体は、他のN-H...O相互作用によってx方向に沿って積重して連結される、最後に、積み重なりは、3種類目のN-H...O相互作用によって、[0 1 1]方向に沿って層状に連結される。 Referring to FIG. 14B, RejuAgro B molecules in the crystal are NH. .. .. The O interaction forms a centrosymmetric H-bonded dimer. These dimers are similar to other N-H. .. .. Finally, the stack is a third type of NH. .. .. Due to the O interaction, they are connected in a layered manner along the [0 1 1] direction.
RejuAgro Bの化学構造は以下に示される: The chemical structure of RejuAgro B is shown below:
RejuAgro B分子の追加の結晶学的データは、表22~29に示される。 Additional crystallographic data for RejuAgro B molecules are shown in Tables 22-29.
C.RejuAgro Cの結晶構造情報
RejuAgro C(C10H16N2O7)の単結晶は、RejuAgro B及びRejuAgro Cのメタノール溶液をゆっくり蒸発させることによって得られた。RejuAgro Bに伴って無色針状が得られた。適当な結晶が選択され、SuperNova、Dual、Cu ホーム/近傍、Atlas回折計に装着された。データ収集中、結晶は100.05(10)Kに保たれた。Olex2(Dolomanovら、(2009))を用いて、構造はCharge Flippingを用いたolex2.solve構造解決プログラム(Bourhisら、(2015))によって解かれ、最小二乗法による最小化を用いたShelXL精密化パッケージ(Sheldrick(2015))によって精密化された。
C. Crystal structure information of RejuAgro C Single crystals of RejuAgro C (C 10 H 16 N 2 O 7 ) were obtained by slowly evaporating methanol solutions of RejuAgro B and RejuAgro C. With RejuAgro B, colorless needles were obtained. A suitable crystal was selected and mounted on a SuperNova, Dual, Cu home/nearby, Atlas diffractometer. The crystal was held at 100.05 (10) K during data collection. Using Olex2 (Dolomanov et al. (2009)), the structure was modified using Charge Flipping. Solved with the solve structure solving program (Bourhis et al. (2015)) and refined with the ShelXL refinement package (Sheldrick (2015)) using least squares minimization.
データセットは、Cu(Kα)放射線を用いたOxford SuperNova回折計で100Kで収集された。 Data sets were collected at 100K on an Oxford SuperNova diffractometer using Cu (Kα) radiation.
RejuAgro C(C10H16N2O7)(M=276.25g/モル)の結晶データ:三斜晶、空間群P-1(2番)、a=7.0334(4)Å、b=10.2354(7)Å、c=10.4693(7)Å、α=116.426(7)°、β=104.722(5)°、γ=97.680(5)°、V=625.72(8)Å3、Z=2、T=100.00(10)K、μ(CuKα)=1.081mm-1、Dcalc=1.466g/cm3、7480反射を測定(10.068°≦2Θ≦140.528°)、2353独立(Rint=0.0405、Rsigma=0.0373)これらはすべての計算で使用された。最終のR1は0.0504(I>2σ(I))、wR2は0.1388(全データ)であった。 Crystal data of RejuAgro C (C 10 H 16 N 2 O 7 ) (M=276.25 g/mol): triclinic, space group P-1 (no. 2), a=7.0334 (4) Å, b = 10.2354 (7) Å, c = 10.4693 (7) Å, α = 116.426 (7) °, β = 104.722 (5) °, γ = 97.680 (5) °, V = 625.72 (8) Å 3 , Z = 2, T = 100.00 (10) K, μ (CuKα) = 1.081 mm −1 , Dcalc = 1.466 g/cm 3 , 7480 reflection measured (10 .068°≦2Θ≦140.528°), 2353 independent (R int =0.0405, R sigma =0.0373), which were used in all calculations. The final R 1 was 0.0504 (I>2σ(I)) and wR 2 was 0.1388 (all data).
精密化モデルの記述は、Olex2で作成され、2018年5月29日にOlexSysのsvn.r3508にコンパイルされた。抑制数-0、拘束数-不明。詳細:1.固定Uiso:1.5倍:全C(H,H,H)基、2.a回転基として精密化した理想化Me:
C9(H9A,H9B,H9C),C10(H10A,H10B,H10C)
The description of the refined model was created in Olex2 and published on May 29, 2018 in OlexSys svn. Compiled to r3508. Number of restraints - 0, number of restraints - unknown. Details: 1. Fixed Uiso: 1.5 times: all C (H, H, H) groups, 2. Idealized Me refined as a rotation group:
C9 (H9A, H9B, H9C), C10 (H10A, H10B, H10C)
図15Aを参照すると、RejuAgro C分子は、アミド基が他の原子の平面から42°回転したπ共役の平面形状を持つ。 Referring to FIG. 15A, the RejuAgro C molecule has a π-conjugated planar shape in which the amide group is rotated by 42° from the plane of other atoms.
図15Bを参照すると、結晶中のRejuAgro C分子は、x軸に沿って積み重なる。この積み重なりは、N-H...OのH結合によってab平面に沿って層になるように接続されている。この層は、複数の水素結合を介して、溶媒和化合物である水分子(3モル当量)と3次元ネットワークに接続されている。 Referring to FIG. 15B, RejuAgro C molecules in the crystal are stacked along the x-axis. This stack is N-H. .. .. They are connected in layers along the ab plane by O H bonds. This layer is connected in a three-dimensional network with solvated water molecules (3 molar equivalents) via multiple hydrogen bonds.
RejuAgro Cの化学構造は以下に示される: The chemical structure of RejuAgro C is shown below:
RejuAgro C分子の追加の結晶学的データは、表30~37に示される。 Additional crystallographic data for RejuAgro C molecules are shown in Tables 30-37.
参照による組み込み
ここで引用されているすべての文献、出版物、特許、特許出願及び関連資料は、本明細書に完全に記載されているかのように参照により組み込まれる。
INCORPORATION BY REFERENCE All documents, publications, patents, patent applications, and related materials cited herein are incorporated by reference as if fully set forth herein.
生物寄託情報
本発明者らのうちの1人である、Ching-Hong Yang博士(アメリカ合衆国、ウィスコンシン・53902、メクォン、ノース・シェリダン・ドライブ・10120在住)は、PCT第13規則の2に基づく「寄託された微生物に関する表示」(PCT/RO/134)(本願において提出)によって証明される、細菌株シュードモナス・ソリ 0617-T307、シュードモナス・ソリ 0917-T305、シュードモナス・ソリ 0917-T306、シュードモナス・ソリ 0917-T307、シュードモナス・モッセリイ 0118-T319、シュードモナス・モッセリイ 0318-T327、及びシュードモナス・モッセリイ 0418-T328を、American Type Culture Collection(ATCC(登録商標))、P.O. Box 1549、 Manassas、VA 20110 USA(「ATCC特許寄託機構」)に2020年6月25日に提出した。生存率試験後、ATCC特許寄託機構は、これらの寄託された細菌株に、2020年6月25日から有効な以下の受託番号を付与した:シュードモナス・ソリ 0617-T307(受託番号PTA-126796)、シュードモナス・ソリ 0917-T305(受託番号PTA-126797)、シュードモナス・ソリ 0917-T306(受託番号PTA-126798)、シュードモナス・ソリ 0917-T307(受託番号PTA-126799)、シュードモナス・モッセリイ 0118-T319(受託番号PTA-126800)、シュードモナス・モッセリイ 0318-T327(受託番号PTA-126801)及びシュードモナス・モッセリイ 0418-T328(受託番号PTA-126802)。Yang博士は、本出願人に対し、この生物寄託の開示を本出願に含めることへの許可を与え、かつ、出願日の時点で公衆に利用可能にされることについて、無条件かつ取消不能な同意を与えている。
Biological deposit information
Dr. Ching-Hong Yang, one of the inventors, of 10120 North Sheridan Drive, Mequon, Wisconsin 53902, United States of America, is the author of the Bacterial strains Pseudomonas sori 0617-T307, Pseudomonas sori 0917-T305 , Pseudomonas sori 0917-T306, Pseudomonas sori 0917-T307, Pseudomonas mosselii 0118-T319, Pseudomonas mosselii 0318-T327, and Pseudomonas mosselii 0418-T328 were purchased from the American Type Culture Collection (ATCC®), P. mosselii. O. Box 1549, Manassas, VA 20110 USA (the ``ATCC Patent Depository'') on June 25, 2020 . After viability testing, the ATCC Patent depository has assigned these deposited bacterial strains the following accession number, effective June 25, 2020: Pseudomonas sori 0617-T307 (Accession number PTA-126796) , Pseudomonas sori 0917-T305 (accession number PTA-126797), Pseudomonas sori 0917-T306 (accession number PTA-126798), Pseudomonas sori 0917-T307 (accession number PTA-126799), Pseudomonas mosselii 0118-T319 ( Accession number PTA-126800), Pseudomonas mosselii 0318-T327 (Accession number PTA-126801), and Pseudomonas mosseri 0418-T328 (Accession number PTA-126802). Dr. Yang hereby unconditionally and irrevocably grants applicant permission to include the disclosure of this biological deposit in this application and to make it available to the public as of the filing date. giving consent.
Claims (53)
i.容器中の液体培地中でシュードモナス(Pseudomonas)属細菌を増殖させて、細菌発酵物を生産するステップであって、培地体積と容器体積の比が約1:2~1:10の間であり、容器が約100~250RPMの間の速度で振盪されるステップ、
又は
ii.発酵槽中の液体培地中でシュードモナス属細菌を増殖させて、細菌発酵物を生産するステップであって、発酵槽の空気流量が約1~3L/分の間であるステップ
を含む方法。 A method of growing bacteria to promote production of protective metabolites, the method comprising:
i. growing Pseudomonas bacteria in a liquid medium in a container to produce a bacterial ferment, the ratio of medium volume to container volume being between about 1:2 and 1:10; shaking the container at a speed between about 100 and 250 RPM;
or ii. A method of growing Pseudomonas bacteria in a liquid medium in a fermenter to produce a bacterial fermentation, the method comprising the steps of: growing Pseudomonas bacteria in a liquid medium in a fermenter, the air flow rate of the fermenter being between about 1 and 3 L/min.
i.請求項1~18のいずれか一項によって生産された細菌発酵物若しくは保護上清を含む農業用組成物、又は請求項19~27のいずれか一項の農業用組成物を生産するステップ;及び
ii.前記農業用組成物を作物に適用して病原微生物の増殖を抑制するステップ、
を含む方法。 1. A method for controlling bacterial crop diseases, the method comprising:
i. producing an agricultural composition comprising the bacterial fermentation or protected supernatant produced according to any one of claims 1 to 18, or an agricultural composition according to any one of claims 19 to 27; and ii. applying the agricultural composition to crops to inhibit the growth of pathogenic microorganisms;
method including.
約1.0×105~1.0×109cfu/mLの間のシュードモナス属細菌を含む農業用組成物を作物に適用して、病原微生物の増殖を抑制すること
を含む方法。 1. A method for controlling bacterial crop diseases, the method comprising:
A method comprising applying to a crop an agricultural composition comprising between about 1.0×10 5 and 1.0×10 9 cfu/mL of Pseudomonas bacteria to inhibit growth of pathogenic microorganisms.
i.請求項1~17のいずれか一項の方法によって細菌発酵物又は保護上清を生産すること、又は請求項18~20のいずれか一項によって生産されるそれらの製剤を生産すること、
ii.酢酸エチル抽出によって、細菌発酵物又は保護上清を抽出すること;並びに
iii.細菌発酵物又は保護上清を50%ヘキサン及び50%酢酸エチルを用いて溶出することにより、又は細菌発酵物又は保護上清を25%ヘキサン及び75%酢酸エチルを用いて溶出することにより、保護代謝物を含む溶出液を生産すること、
を含む方法。 A method for purifying a protected metabolite derived from a Pseudomonas bacterium, the method comprising:
i. producing a bacterial fermentation or a protected supernatant by the method of any one of claims 1 to 17, or a formulation thereof produced according to any one of claims 18 to 20;
ii. Extracting the bacterial fermentation or protected supernatant by ethyl acetate extraction; and iii. Protection by eluting the bacterial fermentation or protected supernatant with 50% hexane and 50% ethyl acetate, or by eluting the bacterial fermentation or protected supernatant with 25% hexane and 75% ethyl acetate. producing an eluate containing the metabolite;
method including.
i.請求項33及び34のいずれか一項の方法により精製されたシュードモナス属細菌由来の保護代謝物を含む農業用組成物を生産すること、及び
ii.前記農業用組成物を作物に適用して、病原微生物の増殖を抑制すること
を含む方法。 1. A method for controlling bacterial crop diseases, the method comprising:
i. producing an agricultural composition comprising a protected metabolite derived from a Pseudomonas bacterium purified by the method of any one of claims 33 and 34; and ii. A method comprising applying the agricultural composition to a crop to inhibit the growth of pathogenic microorganisms.
Applications Claiming Priority (1)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| PCT/US2020/054303 WO2022075969A1 (en) | 2020-10-05 | 2020-10-05 | Pseudomonas strains and their metabolites to control plant diseases |
Publications (1)
| Publication Number | Publication Date |
|---|---|
| JP2023553190A true JP2023553190A (en) | 2023-12-20 |
Family
ID=73198431
Family Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2023545726A Pending JP2023553190A (en) | 2020-10-05 | 2020-10-05 | Pseudomonas strains and their metabolites that control plant diseases |
Country Status (7)
| Country | Link |
|---|---|
| EP (1) | EP4225892A1 (en) |
| JP (1) | JP2023553190A (en) |
| KR (1) | KR20230079416A (en) |
| CN (1) | CN116367723A (en) |
| CA (1) | CA3200796A1 (en) |
| MX (1) | MX2023004043A (en) |
| WO (1) | WO2022075969A1 (en) |
Families Citing this family (2)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| CN115747094B (en) * | 2022-08-30 | 2024-04-02 | 内蒙古农业大学 | Composite bacterial strain composition and application thereof |
| CN116694531B (en) * | 2023-06-29 | 2024-04-05 | 四川农业大学 | Bacillus HLH_19 and application thereof |
Family Cites Families (3)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| BRPI0818478A2 (en) | 2007-10-30 | 2015-04-14 | Veridex Llc | Process for predicting squamous cell lung cancer prognosis |
| AR090186A1 (en) * | 2012-02-28 | 2014-10-22 | Marrone Bio Innovations Inc | CONTROL OF PHYTOOPATHOGENIC MICROORGANISMS WITH PSEUDOMONAS SP. AND SUBSTANCES AND COMPOSITIONS DERIVED FROM THE SAME |
| EP3941205A1 (en) * | 2019-03-18 | 2022-01-26 | Futureco Bioscience, S.A. | Pseudomonas sp. strain, composition comprising the same, and uses thereof |
-
2020
- 2020-10-05 WO PCT/US2020/054303 patent/WO2022075969A1/en unknown
- 2020-10-05 JP JP2023545726A patent/JP2023553190A/en active Pending
- 2020-10-05 EP EP20804015.4A patent/EP4225892A1/en active Pending
- 2020-10-05 MX MX2023004043A patent/MX2023004043A/en unknown
- 2020-10-05 CA CA3200796A patent/CA3200796A1/en active Pending
- 2020-10-05 KR KR1020237014746A patent/KR20230079416A/en unknown
- 2020-10-05 CN CN202080105958.0A patent/CN116367723A/en active Pending
Also Published As
| Publication number | Publication date |
|---|---|
| KR20230079416A (en) | 2023-06-07 |
| EP4225892A1 (en) | 2023-08-16 |
| CN116367723A (en) | 2023-06-30 |
| WO2022075969A1 (en) | 2022-04-14 |
| MX2023004043A (en) | 2023-08-22 |
| CA3200796A1 (en) | 2022-04-14 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| Le et al. | Biological control of tomato bacterial wilt, kimchi cabbage soft rot, and red pepper bacterial leaf spot using Paenibacillus elgii JCK-5075 | |
| EP1788074B1 (en) | Novel strains belonging to the genus paenibacillus and method of controlling plant disease by using these strains or culture thereof | |
| KR101904473B1 (en) | Bacillus methylotrophicus DR-08 strain producing natural volatile compound and having antimicrobial activity and uses thereof | |
| US20230165260A1 (en) | Pseudomonas strains and their metabolites to control plant diseases | |
| KR101971017B1 (en) | Bacillus methylotrophicus 8-2 strain producing natural volatile compound and having antimicrobial activity | |
| KR102375337B1 (en) | Composition for controlling plant diseases using Brevibacillus brevis HK544 | |
| BG105982A (en) | A STRAIN OF i(BACILLUS) PUMILUS FOR CONTROLLING PLANT DISEASES | |
| US7387888B2 (en) | Coronamycins | |
| US12089595B2 (en) | Pseudomonas strains and their metabolites to control plant diseases | |
| JP2023553190A (en) | Pseudomonas strains and their metabolites that control plant diseases | |
| JP2023546531A (en) | Pseudomonas strains and their metabolites that control plant diseases | |
| WO2014065589A1 (en) | Lysinibacillus sphaericus tc1 strain, microbial preparation for controlling plant diseases comprising said strain, and plant disease control method using same | |
| WO2007120253A2 (en) | Endophytic streptomycetes, compounds derived therefrom, and methods of their use | |
| KR101131563B1 (en) | Novel bacterium Bacillus subtilis S1, novel peptides from it and use thereof | |
| KR101152671B1 (en) | A novel strain of Bacillus sp. BS061 having anti-pathogens activity and composition for controlling plant disease | |
| CN114380782A (en) | Compound, preparation method and application of bactericide in preventing and treating rubber anthracnose | |
| KR100319135B1 (en) | Microbiological preparation inhibiting plant diseases | |
| TW202214837A (en) | Pseudomonas strains and their metabolites to control plant diseases | |
| CN116648139A (en) | Pseudomonas strain for controlling plant diseases and metabolite thereof | |
| KR101418492B1 (en) | Novel mannosyl lipid derivatives derived from Simplicillium lamellicola KRICT3 and composition containing the same for control plant diseases or insects | |
| KR101956833B1 (en) | Lysinibacillus sphaericus tc1 strain and method for controlling plant diseases using the same |
Legal Events
| Date | Code | Title | Description |
|---|---|---|---|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20230606 |
|
| A621 | Written request for application examination |
Free format text: JAPANESE INTERMEDIATE CODE: A621 Effective date: 20230919 |