JP2023519871A - Stmn2レベルを回復させるための方法及び組成物 - Google Patents
Stmn2レベルを回復させるための方法及び組成物 Download PDFInfo
- Publication number
- JP2023519871A JP2023519871A JP2022558277A JP2022558277A JP2023519871A JP 2023519871 A JP2023519871 A JP 2023519871A JP 2022558277 A JP2022558277 A JP 2022558277A JP 2022558277 A JP2022558277 A JP 2022558277A JP 2023519871 A JP2023519871 A JP 2023519871A
- Authority
- JP
- Japan
- Prior art keywords
- stmn2
- tdp
- seq
- disease
- site
- Prior art date
- Legal status (The legal status is an assumption and is not a legal conclusion. Google has not performed a legal analysis and makes no representation as to the accuracy of the status listed.)
- Pending
Links
- 101000697510 Homo sapiens Stathmin-2 Proteins 0.000 title claims abstract description 574
- 102100028051 Stathmin-2 Human genes 0.000 title claims abstract description 571
- 238000000034 method Methods 0.000 title claims abstract description 152
- 239000000203 mixture Substances 0.000 title claims abstract description 27
- 102100040347 TAR DNA-binding protein 43 Human genes 0.000 claims abstract description 495
- 101710150875 TAR DNA-binding protein 43 Proteins 0.000 claims abstract description 474
- 108091032973 (ribonucleotides)n+m Proteins 0.000 claims abstract description 168
- 210000002569 neuron Anatomy 0.000 claims abstract description 111
- 208000037265 diseases, disorders, signs and symptoms Diseases 0.000 claims abstract description 108
- 201000010099 disease Diseases 0.000 claims abstract description 97
- 230000003247 decreasing effect Effects 0.000 claims abstract description 28
- 230000003902 lesion Effects 0.000 claims abstract description 14
- 230000002950 deficient Effects 0.000 claims abstract description 9
- 230000002401 inhibitory effect Effects 0.000 claims abstract description 7
- 239000000074 antisense oligonucleotide Substances 0.000 claims description 293
- 238000012230 antisense oligonucleotides Methods 0.000 claims description 293
- 108091034117 Oligonucleotide Proteins 0.000 claims description 218
- 206010002026 amyotrophic lateral sclerosis Diseases 0.000 claims description 174
- 239000003795 chemical substances by application Substances 0.000 claims description 157
- 108020000948 Antisense Oligonucleotides Proteins 0.000 claims description 139
- 230000014509 gene expression Effects 0.000 claims description 98
- 108700024394 Exon Proteins 0.000 claims description 83
- 108020004999 messenger RNA Proteins 0.000 claims description 82
- 230000008488 polyadenylation Effects 0.000 claims description 79
- 230000027455 binding Effects 0.000 claims description 78
- 108020005067 RNA Splice Sites Proteins 0.000 claims description 74
- 239000008194 pharmaceutical composition Substances 0.000 claims description 65
- 230000002829 reductive effect Effects 0.000 claims description 64
- 208000015122 neurodegenerative disease Diseases 0.000 claims description 45
- 201000011240 Frontotemporal dementia Diseases 0.000 claims description 44
- 208000030886 Traumatic Brain injury Diseases 0.000 claims description 44
- 102000007301 ELAV-Like Protein 3 Human genes 0.000 claims description 43
- 239000000523 sample Substances 0.000 claims description 43
- 108010008796 ELAV-Like Protein 3 Proteins 0.000 claims description 42
- 230000009529 traumatic brain injury Effects 0.000 claims description 42
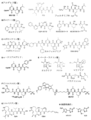
- JLCPHMBAVCMARE-UHFFFAOYSA-N [3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-[[3-[[3-[[3-[[3-[[3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-hydroxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methyl [5-(6-aminopurin-9-yl)-2-(hydroxymethyl)oxolan-3-yl] hydrogen phosphate Polymers Cc1cn(C2CC(OP(O)(=O)OCC3OC(CC3OP(O)(=O)OCC3OC(CC3O)n3cnc4c3nc(N)[nH]c4=O)n3cnc4c3nc(N)[nH]c4=O)C(COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3CO)n3cnc4c(N)ncnc34)n3ccc(N)nc3=O)n3cnc4c(N)ncnc34)n3ccc(N)nc3=O)n3ccc(N)nc3=O)n3ccc(N)nc3=O)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cc(C)c(=O)[nH]c3=O)n3cc(C)c(=O)[nH]c3=O)n3ccc(N)nc3=O)n3cc(C)c(=O)[nH]c3=O)n3cnc4c3nc(N)[nH]c4=O)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)O2)c(=O)[nH]c1=O JLCPHMBAVCMARE-UHFFFAOYSA-N 0.000 claims description 38
- 230000001965 increasing effect Effects 0.000 claims description 36
- 230000004770 neurodegeneration Effects 0.000 claims description 33
- 230000001105 regulatory effect Effects 0.000 claims description 31
- 125000003729 nucleotide group Chemical group 0.000 claims description 23
- 208000024827 Alzheimer disease Diseases 0.000 claims description 19
- 208000018737 Parkinson disease Diseases 0.000 claims description 18
- 108091028043 Nucleic acid sequence Proteins 0.000 claims description 14
- 230000007514 neuronal growth Effects 0.000 claims description 14
- 230000007823 neuropathy Effects 0.000 claims description 14
- 201000001119 neuropathy Diseases 0.000 claims description 14
- 208000033808 peripheral neuropathy Diseases 0.000 claims description 14
- 230000008439 repair process Effects 0.000 claims description 14
- 229940079156 Proteasome inhibitor Drugs 0.000 claims description 13
- 239000003207 proteasome inhibitor Substances 0.000 claims description 13
- 239000012825 JNK inhibitor Substances 0.000 claims description 12
- 229940118135 JNK inhibitor Drugs 0.000 claims description 12
- 230000003292 diminished effect Effects 0.000 claims description 12
- 239000002773 nucleotide Substances 0.000 claims description 11
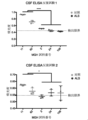
- 238000002965 ELISA Methods 0.000 claims description 10
- 201000008319 inclusion body myositis Diseases 0.000 claims description 9
- 239000013060 biological fluid Substances 0.000 claims description 8
- 210000003061 neural cell Anatomy 0.000 claims description 8
- 230000008859 change Effects 0.000 claims description 7
- 238000001415 gene therapy Methods 0.000 claims description 7
- 230000001976 improved effect Effects 0.000 claims description 5
- 230000000692 anti-sense effect Effects 0.000 claims 2
- 239000013074 reference sample Substances 0.000 claims 1
- 210000004027 cell Anatomy 0.000 description 137
- 108090000623 proteins and genes Proteins 0.000 description 104
- 210000002161 motor neuron Anatomy 0.000 description 99
- 238000004458 analytical method Methods 0.000 description 68
- 238000011282 treatment Methods 0.000 description 52
- 108020004459 Small interfering RNA Proteins 0.000 description 49
- 238000003559 RNA-seq method Methods 0.000 description 48
- 102000004169 proteins and genes Human genes 0.000 description 43
- 210000001175 cerebrospinal fluid Anatomy 0.000 description 40
- 230000006870 function Effects 0.000 description 39
- 230000035772 mutation Effects 0.000 description 37
- 235000018102 proteins Nutrition 0.000 description 35
- 238000011870 unpaired t-test Methods 0.000 description 34
- 102000004245 Proteasome Endopeptidase Complex Human genes 0.000 description 32
- 108090000708 Proteasome Endopeptidase Complex Proteins 0.000 description 32
- 230000009467 reduction Effects 0.000 description 32
- 235000000346 sugar Nutrition 0.000 description 32
- 238000011529 RT qPCR Methods 0.000 description 31
- 230000003376 axonal effect Effects 0.000 description 29
- 230000005764 inhibitory process Effects 0.000 description 28
- 238000003556 assay Methods 0.000 description 25
- 230000000694 effects Effects 0.000 description 23
- 230000008685 targeting Effects 0.000 description 23
- 238000002474 experimental method Methods 0.000 description 22
- 230000001537 neural effect Effects 0.000 description 22
- 238000012360 testing method Methods 0.000 description 22
- 210000000130 stem cell Anatomy 0.000 description 21
- 208000027418 Wounds and injury Diseases 0.000 description 18
- 230000006378 damage Effects 0.000 description 18
- 208000014674 injury Diseases 0.000 description 18
- 230000014511 neuron projection development Effects 0.000 description 18
- 238000012216 screening Methods 0.000 description 18
- 238000012217 deletion Methods 0.000 description 17
- 230000037430 deletion Effects 0.000 description 17
- 238000003119 immunoblot Methods 0.000 description 17
- 230000004069 differentiation Effects 0.000 description 16
- 230000004807 localization Effects 0.000 description 16
- 239000002609 medium Substances 0.000 description 16
- 210000001519 tissue Anatomy 0.000 description 16
- FWBHETKCLVMNFS-UHFFFAOYSA-N 4',6-Diamino-2-phenylindol Chemical compound C1=CC(C(=N)N)=CC=C1C1=CC2=CC=C(C(N)=N)C=C2N1 FWBHETKCLVMNFS-UHFFFAOYSA-N 0.000 description 15
- WSFSSNUMVMOOMR-UHFFFAOYSA-N Formaldehyde Chemical compound O=C WSFSSNUMVMOOMR-UHFFFAOYSA-N 0.000 description 15
- 230000003828 downregulation Effects 0.000 description 15
- 230000004048 modification Effects 0.000 description 15
- 238000012986 modification Methods 0.000 description 15
- 239000013610 patient sample Substances 0.000 description 15
- 108091033409 CRISPR Proteins 0.000 description 14
- 101000891092 Homo sapiens TAR DNA-binding protein 43 Proteins 0.000 description 14
- 102000004243 Tubulin Human genes 0.000 description 14
- 108090000704 Tubulin Proteins 0.000 description 14
- 230000002776 aggregation Effects 0.000 description 14
- 238000004220 aggregation Methods 0.000 description 14
- 230000033228 biological regulation Effects 0.000 description 14
- 102000003890 RNA-binding protein FUS Human genes 0.000 description 13
- 108090000292 RNA-binding protein FUS Proteins 0.000 description 13
- 210000003050 axon Anatomy 0.000 description 13
- 125000003835 nucleoside group Chemical group 0.000 description 13
- 102000009664 Microtubule-Associated Proteins Human genes 0.000 description 12
- 108010012715 Superoxide dismutase Proteins 0.000 description 12
- 238000011069 regeneration method Methods 0.000 description 12
- 238000012163 sequencing technique Methods 0.000 description 12
- 150000003384 small molecules Chemical class 0.000 description 12
- 238000001890 transfection Methods 0.000 description 12
- 238000010354 CRISPR gene editing Methods 0.000 description 11
- 108010020004 Microtubule-Associated Proteins Proteins 0.000 description 11
- 102000019197 Superoxide Dismutase Human genes 0.000 description 11
- 210000002241 neurite Anatomy 0.000 description 11
- 230000008929 regeneration Effects 0.000 description 11
- 210000000278 spinal cord Anatomy 0.000 description 11
- 230000035882 stress Effects 0.000 description 11
- 101000665442 Homo sapiens Serine/threonine-protein kinase TBK1 Proteins 0.000 description 10
- 108010055717 JNK Mitogen-Activated Protein Kinases Proteins 0.000 description 10
- 241001465754 Metazoa Species 0.000 description 10
- 241000699670 Mus sp. Species 0.000 description 10
- 102100038192 Serine/threonine-protein kinase TBK1 Human genes 0.000 description 10
- 108050003387 Stathmin Proteins 0.000 description 10
- 230000015572 biosynthetic process Effects 0.000 description 10
- 208000035475 disorder Diseases 0.000 description 10
- 239000003814 drug Substances 0.000 description 10
- 239000003112 inhibitor Substances 0.000 description 10
- 210000005230 lumbar spinal cord Anatomy 0.000 description 10
- 230000007246 mechanism Effects 0.000 description 10
- 230000001404 mediated effect Effects 0.000 description 10
- 230000001575 pathological effect Effects 0.000 description 10
- 239000000047 product Substances 0.000 description 10
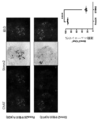
- 238000010186 staining Methods 0.000 description 10
- 239000000126 substance Substances 0.000 description 10
- 102000040650 (ribonucleotides)n+m Human genes 0.000 description 9
- 108020004414 DNA Proteins 0.000 description 9
- 102000029749 Microtubule Human genes 0.000 description 9
- 108091022875 Microtubule Proteins 0.000 description 9
- 102000005465 Stathmin Human genes 0.000 description 9
- 125000002619 bicyclic group Chemical group 0.000 description 9
- 210000004556 brain Anatomy 0.000 description 9
- 230000015556 catabolic process Effects 0.000 description 9
- 238000006731 degradation reaction Methods 0.000 description 9
- 235000019688 fish Nutrition 0.000 description 9
- 238000001943 fluorescence-activated cell sorting Methods 0.000 description 9
- 239000008187 granular material Substances 0.000 description 9
- 238000001727 in vivo Methods 0.000 description 9
- 210000004688 microtubule Anatomy 0.000 description 9
- 230000037361 pathway Effects 0.000 description 9
- 230000004044 response Effects 0.000 description 9
- 238000003757 reverse transcription PCR Methods 0.000 description 9
- 108020005004 Guide RNA Proteins 0.000 description 8
- 102100024392 Insulin gene enhancer protein ISL-1 Human genes 0.000 description 8
- 108010069196 Neural Cell Adhesion Molecules Proteins 0.000 description 8
- 102100027347 Neural cell adhesion molecule 1 Human genes 0.000 description 8
- 108091030071 RNAI Proteins 0.000 description 8
- 238000000692 Student's t-test Methods 0.000 description 8
- 239000000090 biomarker Substances 0.000 description 8
- 239000000872 buffer Substances 0.000 description 8
- 230000001086 cytosolic effect Effects 0.000 description 8
- 230000007423 decrease Effects 0.000 description 8
- 238000002509 fluorescent in situ hybridization Methods 0.000 description 8
- 230000012010 growth Effects 0.000 description 8
- 238000000338 in vitro Methods 0.000 description 8
- 210000004498 neuroglial cell Anatomy 0.000 description 8
- 108090000765 processed proteins & peptides Proteins 0.000 description 8
- 238000011002 quantification Methods 0.000 description 8
- 239000011435 rock Substances 0.000 description 8
- 238000003118 sandwich ELISA Methods 0.000 description 8
- 239000000243 solution Substances 0.000 description 8
- 125000001424 substituent group Chemical group 0.000 description 8
- 208000024891 symptom Diseases 0.000 description 8
- 239000013598 vector Substances 0.000 description 8
- 230000035508 accumulation Effects 0.000 description 7
- 238000009825 accumulation Methods 0.000 description 7
- SHGAZHPCJJPHSC-YCNIQYBTSA-N all-trans-retinoic acid Chemical compound OC(=O)\C=C(/C)\C=C\C=C(/C)\C=C\C1=C(C)CCCC1(C)C SHGAZHPCJJPHSC-YCNIQYBTSA-N 0.000 description 7
- 238000013459 approach Methods 0.000 description 7
- -1 but not limited to Chemical group 0.000 description 7
- 230000001413 cellular effect Effects 0.000 description 7
- 210000003169 central nervous system Anatomy 0.000 description 7
- 230000006735 deficit Effects 0.000 description 7
- 230000007850 degeneration Effects 0.000 description 7
- 230000009368 gene silencing by RNA Effects 0.000 description 7
- 208000005264 motor neuron disease Diseases 0.000 description 7
- 102000039446 nucleic acids Human genes 0.000 description 7
- 108020004707 nucleic acids Proteins 0.000 description 7
- 150000007523 nucleic acids Chemical class 0.000 description 7
- 239000002777 nucleoside Substances 0.000 description 7
- 230000036961 partial effect Effects 0.000 description 7
- 210000001778 pluripotent stem cell Anatomy 0.000 description 7
- 229930002330 retinoic acid Natural products 0.000 description 7
- 125000002652 ribonucleotide group Chemical group 0.000 description 7
- 239000003765 sweetening agent Substances 0.000 description 7
- 238000003786 synthesis reaction Methods 0.000 description 7
- 229960001727 tretinoin Drugs 0.000 description 7
- 238000010200 validation analysis Methods 0.000 description 7
- 208000002339 Frontotemporal Lobar Degeneration Diseases 0.000 description 6
- 102100031181 Glyceraldehyde-3-phosphate dehydrogenase Human genes 0.000 description 6
- XSQUKJJJFZCRTK-UHFFFAOYSA-N Urea Chemical compound NC(N)=O XSQUKJJJFZCRTK-UHFFFAOYSA-N 0.000 description 6
- 239000002299 complementary DNA Substances 0.000 description 6
- 230000007547 defect Effects 0.000 description 6
- 229940079593 drug Drugs 0.000 description 6
- 238000005516 engineering process Methods 0.000 description 6
- 108020004445 glyceraldehyde-3-phosphate dehydrogenase Proteins 0.000 description 6
- 238000003365 immunocytochemistry Methods 0.000 description 6
- 230000006698 induction Effects 0.000 description 6
- 230000007111 proteostasis Effects 0.000 description 6
- RXWNCPJZOCPEPQ-NVWDDTSBSA-N puromycin Chemical compound C1=CC(OC)=CC=C1C[C@H](N)C(=O)N[C@H]1[C@@H](O)[C@H](N2C3=NC=NC(=C3N=C2)N(C)C)O[C@@H]1CO RXWNCPJZOCPEPQ-NVWDDTSBSA-N 0.000 description 6
- 230000011664 signaling Effects 0.000 description 6
- 235000021092 sugar substitutes Nutrition 0.000 description 6
- XLYOFNOQVPJJNP-UHFFFAOYSA-N water Substances O XLYOFNOQVPJJNP-UHFFFAOYSA-N 0.000 description 6
- 238000001262 western blot Methods 0.000 description 6
- 102000004219 Brain-derived neurotrophic factor Human genes 0.000 description 5
- 108090000715 Brain-derived neurotrophic factor Proteins 0.000 description 5
- LFQSCWFLJHTTHZ-UHFFFAOYSA-N Ethanol Chemical compound CCO LFQSCWFLJHTTHZ-UHFFFAOYSA-N 0.000 description 5
- 101001053263 Homo sapiens Insulin gene enhancer protein ISL-1 Proteins 0.000 description 5
- 208000026072 Motor neurone disease Diseases 0.000 description 5
- 241000699666 Mus <mouse, genus> Species 0.000 description 5
- 241000288906 Primates Species 0.000 description 5
- 108010029485 Protein Isoforms Proteins 0.000 description 5
- 102000001708 Protein Isoforms Human genes 0.000 description 5
- 208000029033 Spinal Cord disease Diseases 0.000 description 5
- 101150014554 TARDBP gene Proteins 0.000 description 5
- 229940024606 amino acid Drugs 0.000 description 5
- 230000000903 blocking effect Effects 0.000 description 5
- 210000005056 cell body Anatomy 0.000 description 5
- 238000003570 cell viability assay Methods 0.000 description 5
- 238000010367 cloning Methods 0.000 description 5
- 239000003937 drug carrier Substances 0.000 description 5
- 238000010195 expression analysis Methods 0.000 description 5
- 238000010362 genome editing Methods 0.000 description 5
- 238000003205 genotyping method Methods 0.000 description 5
- 210000000020 growth cone Anatomy 0.000 description 5
- 230000009643 growth defect Effects 0.000 description 5
- 238000001114 immunoprecipitation Methods 0.000 description 5
- 210000004263 induced pluripotent stem cell Anatomy 0.000 description 5
- 239000012528 membrane Substances 0.000 description 5
- 230000004060 metabolic process Effects 0.000 description 5
- 230000007170 pathology Effects 0.000 description 5
- 239000000546 pharmaceutical excipient Substances 0.000 description 5
- 229910052698 phosphorus Inorganic materials 0.000 description 5
- 230000002028 premature Effects 0.000 description 5
- 238000002360 preparation method Methods 0.000 description 5
- 102000004196 processed proteins & peptides Human genes 0.000 description 5
- 238000012545 processing Methods 0.000 description 5
- 238000000746 purification Methods 0.000 description 5
- 238000011160 research Methods 0.000 description 5
- 238000002473 ribonucleic acid immunoprecipitation Methods 0.000 description 5
- 230000000392 somatic effect Effects 0.000 description 5
- 239000000758 substrate Substances 0.000 description 5
- 230000001629 suppression Effects 0.000 description 5
- 230000002103 transcriptional effect Effects 0.000 description 5
- 230000032258 transport Effects 0.000 description 5
- IDDDVXIUIXWAGJ-DDSAHXNVSA-N 4-[(1r)-1-aminoethyl]-n-pyridin-4-ylcyclohexane-1-carboxamide;dihydrochloride Chemical compound Cl.Cl.C1CC([C@H](N)C)CCC1C(=O)NC1=CC=NC=C1 IDDDVXIUIXWAGJ-DDSAHXNVSA-N 0.000 description 4
- PEHVGBZKEYRQSX-UHFFFAOYSA-N 7-deaza-adenine Chemical compound NC1=NC=NC2=C1C=CN2 PEHVGBZKEYRQSX-UHFFFAOYSA-N 0.000 description 4
- 101150001232 ALS gene Proteins 0.000 description 4
- IGAZHQIYONOHQN-UHFFFAOYSA-N Alexa Fluor 555 Chemical compound C=12C=CC(=N)C(S(O)(=O)=O)=C2OC2=C(S(O)(=O)=O)C(N)=CC=C2C=1C1=CC=C(C(O)=O)C=C1C(O)=O IGAZHQIYONOHQN-UHFFFAOYSA-N 0.000 description 4
- 108010005939 Ciliary Neurotrophic Factor Proteins 0.000 description 4
- 102100031614 Ciliary neurotrophic factor Human genes 0.000 description 4
- 102000034615 Glial cell line-derived neurotrophic factor Human genes 0.000 description 4
- 108091010837 Glial cell line-derived neurotrophic factor Proteins 0.000 description 4
- 241000282412 Homo Species 0.000 description 4
- 101000697502 Homo sapiens Stathmin-3 Proteins 0.000 description 4
- TWRXJAOTZQYOKJ-UHFFFAOYSA-L Magnesium chloride Chemical compound [Mg+2].[Cl-].[Cl-] TWRXJAOTZQYOKJ-UHFFFAOYSA-L 0.000 description 4
- 206010056677 Nerve degeneration Diseases 0.000 description 4
- OAICVXFJPJFONN-UHFFFAOYSA-N Phosphorus Chemical compound [P] OAICVXFJPJFONN-UHFFFAOYSA-N 0.000 description 4
- 108010004729 Phycoerythrin Proteins 0.000 description 4
- 241000283984 Rodentia Species 0.000 description 4
- 101150104529 Stmn2 gene Proteins 0.000 description 4
- VREFGVBLTWBCJP-UHFFFAOYSA-N alprazolam Chemical compound C12=CC(Cl)=CC=C2N2C(C)=NN=C2CN=C1C1=CC=CC=C1 VREFGVBLTWBCJP-UHFFFAOYSA-N 0.000 description 4
- 235000001014 amino acid Nutrition 0.000 description 4
- 150000001413 amino acids Chemical class 0.000 description 4
- 125000004429 atom Chemical group 0.000 description 4
- 210000000349 chromosome Anatomy 0.000 description 4
- 150000001875 compounds Chemical class 0.000 description 4
- 230000006743 cytoplasmic accumulation Effects 0.000 description 4
- 230000001419 dependent effect Effects 0.000 description 4
- 238000011161 development Methods 0.000 description 4
- 230000018109 developmental process Effects 0.000 description 4
- 238000003745 diagnosis Methods 0.000 description 4
- 238000010586 diagram Methods 0.000 description 4
- 238000000684 flow cytometry Methods 0.000 description 4
- 125000003843 furanosyl group Chemical group 0.000 description 4
- 238000010166 immunofluorescence Methods 0.000 description 4
- 238000012744 immunostaining Methods 0.000 description 4
- 230000001771 impaired effect Effects 0.000 description 4
- 238000002347 injection Methods 0.000 description 4
- 239000007924 injection Substances 0.000 description 4
- 238000004519 manufacturing process Methods 0.000 description 4
- 238000005259 measurement Methods 0.000 description 4
- 239000002679 microRNA Substances 0.000 description 4
- 230000008506 pathogenesis Effects 0.000 description 4
- 230000001717 pathogenic effect Effects 0.000 description 4
- 239000011574 phosphorus Substances 0.000 description 4
- 238000007619 statistical method Methods 0.000 description 4
- 238000012353 t test Methods 0.000 description 4
- 230000001225 therapeutic effect Effects 0.000 description 4
- JKMHFZQWWAIEOD-UHFFFAOYSA-N 2-[4-(2-hydroxyethyl)piperazin-1-yl]ethanesulfonic acid Chemical compound OCC[NH+]1CCN(CCS([O-])(=O)=O)CC1 JKMHFZQWWAIEOD-UHFFFAOYSA-N 0.000 description 3
- 206010003694 Atrophy Diseases 0.000 description 3
- 239000012583 B-27 Supplement Substances 0.000 description 3
- 102100027557 Calcipressin-1 Human genes 0.000 description 3
- IAZDPXIOMUYVGZ-UHFFFAOYSA-N Dimethylsulphoxide Chemical compound CS(C)=O IAZDPXIOMUYVGZ-UHFFFAOYSA-N 0.000 description 3
- 102000018651 Epithelial Cell Adhesion Molecule Human genes 0.000 description 3
- 108010066687 Epithelial Cell Adhesion Molecule Proteins 0.000 description 3
- 101100534511 Gekko japonicus STMN1 gene Proteins 0.000 description 3
- DHMQDGOQFOQNFH-UHFFFAOYSA-N Glycine Chemical compound NCC(O)=O DHMQDGOQFOQNFH-UHFFFAOYSA-N 0.000 description 3
- 239000007995 HEPES buffer Substances 0.000 description 3
- 101000580357 Homo sapiens Calcipressin-1 Proteins 0.000 description 3
- 101000589632 Homo sapiens N-acetylaspartate synthetase Proteins 0.000 description 3
- 101001117219 Homo sapiens Polymerase delta-interacting protein 3 Proteins 0.000 description 3
- 101000831940 Homo sapiens Stathmin Proteins 0.000 description 3
- VLSMHEGGTFMBBZ-OOZYFLPDSA-M Kainate Chemical compound CC(=C)[C@H]1C[NH2+][C@H](C([O-])=O)[C@H]1CC([O-])=O VLSMHEGGTFMBBZ-OOZYFLPDSA-M 0.000 description 3
- 108010085895 Laminin Proteins 0.000 description 3
- 239000012580 N-2 Supplement Substances 0.000 description 3
- 102100032380 N-acetylaspartate synthetase Human genes 0.000 description 3
- 101710163270 Nuclease Proteins 0.000 description 3
- 238000010220 Pearson correlation analysis Methods 0.000 description 3
- 239000012083 RIPA buffer Substances 0.000 description 3
- 102000044126 RNA-Binding Proteins Human genes 0.000 description 3
- 108091028664 Ribonucleotide Proteins 0.000 description 3
- FAPWRFPIFSIZLT-UHFFFAOYSA-M Sodium chloride Chemical compound [Na+].[Cl-] FAPWRFPIFSIZLT-UHFFFAOYSA-M 0.000 description 3
- HEMHJVSKTPXQMS-UHFFFAOYSA-M Sodium hydroxide Chemical compound [OH-].[Na+] HEMHJVSKTPXQMS-UHFFFAOYSA-M 0.000 description 3
- 102100024237 Stathmin Human genes 0.000 description 3
- 102000000353 Stathmin-2 Human genes 0.000 description 3
- 108050008927 Stathmin-2 Proteins 0.000 description 3
- 102100028052 Stathmin-3 Human genes 0.000 description 3
- 102100028049 Stathmin-4 Human genes 0.000 description 3
- 208000036278 TDP-43 proteinopathy Diseases 0.000 description 3
- 241000251539 Vertebrata <Metazoa> Species 0.000 description 3
- 230000001594 aberrant effect Effects 0.000 description 3
- 239000000556 agonist Substances 0.000 description 3
- 230000004075 alteration Effects 0.000 description 3
- 230000037444 atrophy Effects 0.000 description 3
- 230000004900 autophagic degradation Effects 0.000 description 3
- 210000005013 brain tissue Anatomy 0.000 description 3
- 239000004202 carbamide Substances 0.000 description 3
- 229910052799 carbon Inorganic materials 0.000 description 3
- 238000012054 celltiter-glo Methods 0.000 description 3
- 238000006243 chemical reaction Methods 0.000 description 3
- 230000009514 concussion Effects 0.000 description 3
- 230000000875 corresponding effect Effects 0.000 description 3
- 238000001514 detection method Methods 0.000 description 3
- 239000003085 diluting agent Substances 0.000 description 3
- 238000010790 dilution Methods 0.000 description 3
- 239000012895 dilution Substances 0.000 description 3
- 235000019441 ethanol Nutrition 0.000 description 3
- 210000001808 exosome Anatomy 0.000 description 3
- 239000000284 extract Substances 0.000 description 3
- 238000009472 formulation Methods 0.000 description 3
- 208000013967 frontotemporal dementia and/or amyotrophic lateral sclerosis 1 Diseases 0.000 description 3
- 230000002068 genetic effect Effects 0.000 description 3
- 102000046472 human STMN2 Human genes 0.000 description 3
- 238000000099 in vitro assay Methods 0.000 description 3
- 238000011534 incubation Methods 0.000 description 3
- 238000001802 infusion Methods 0.000 description 3
- 108010090448 insulin gene enhancer binding protein Isl-1 Proteins 0.000 description 3
- 238000007913 intrathecal administration Methods 0.000 description 3
- 230000028161 membrane depolarization Effects 0.000 description 3
- 230000000626 neurodegenerative effect Effects 0.000 description 3
- 230000007171 neuropathology Effects 0.000 description 3
- 210000004940 nucleus Anatomy 0.000 description 3
- 210000000056 organ Anatomy 0.000 description 3
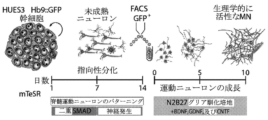
- 238000000059 patterning Methods 0.000 description 3
- 229920001184 polypeptide Polymers 0.000 description 3
- 229950010131 puromycin Drugs 0.000 description 3
- 230000002441 reversible effect Effects 0.000 description 3
- 239000002336 ribonucleotide Substances 0.000 description 3
- 210000002966 serum Anatomy 0.000 description 3
- 241000894007 species Species 0.000 description 3
- 238000013518 transcription Methods 0.000 description 3
- 230000035897 transcription Effects 0.000 description 3
- 238000012795 verification Methods 0.000 description 3
- 238000012800 visualization Methods 0.000 description 3
- FZWGECJQACGGTI-UHFFFAOYSA-N 2-amino-7-methyl-1,7-dihydro-6H-purin-6-one Chemical compound NC1=NC(O)=C2N(C)C=NC2=N1 FZWGECJQACGGTI-UHFFFAOYSA-N 0.000 description 2
- ICSNLGPSRYBMBD-UHFFFAOYSA-N 2-aminopyridine Chemical compound NC1=CC=CC=N1 ICSNLGPSRYBMBD-UHFFFAOYSA-N 0.000 description 2
- OVONXEQGWXGFJD-UHFFFAOYSA-N 4-sulfanylidene-1h-pyrimidin-2-one Chemical compound SC=1C=CNC(=O)N=1 OVONXEQGWXGFJD-UHFFFAOYSA-N 0.000 description 2
- RYVNIFSIEDRLSJ-UHFFFAOYSA-N 5-(hydroxymethyl)cytosine Chemical compound NC=1NC(=O)N=CC=1CO RYVNIFSIEDRLSJ-UHFFFAOYSA-N 0.000 description 2
- HCGHYQLFMPXSDU-UHFFFAOYSA-N 7-methyladenine Chemical compound C1=NC(N)=C2N(C)C=NC2=N1 HCGHYQLFMPXSDU-UHFFFAOYSA-N 0.000 description 2
- 108010082775 97-kDa Golgi complex autoantigen Proteins 0.000 description 2
- MSSXOMSJDRHRMC-UHFFFAOYSA-N 9H-purine-2,6-diamine Chemical compound NC1=NC(N)=C2NC=NC2=N1 MSSXOMSJDRHRMC-UHFFFAOYSA-N 0.000 description 2
- LRFVTYWOQMYALW-UHFFFAOYSA-N 9H-xanthine Chemical compound O=C1NC(=O)NC2=C1NC=N2 LRFVTYWOQMYALW-UHFFFAOYSA-N 0.000 description 2
- 102100025514 ATP-dependent 6-phosphofructokinase, platelet type Human genes 0.000 description 2
- 101710159080 Aconitate hydratase A Proteins 0.000 description 2
- 101710159078 Aconitate hydratase B Proteins 0.000 description 2
- 229920001817 Agar Polymers 0.000 description 2
- HJCMDXDYPOUFDY-WHFBIAKZSA-N Ala-Gln Chemical compound C[C@H](N)C(=O)N[C@H](C(O)=O)CCC(N)=O HJCMDXDYPOUFDY-WHFBIAKZSA-N 0.000 description 2
- 239000012117 Alexa Fluor 700 Substances 0.000 description 2
- 208000031277 Amaurotic familial idiocy Diseases 0.000 description 2
- 108020005544 Antisense RNA Proteins 0.000 description 2
- 108091023037 Aptamer Proteins 0.000 description 2
- IJGRMHOSHXDMSA-UHFFFAOYSA-N Atomic nitrogen Chemical compound N#N IJGRMHOSHXDMSA-UHFFFAOYSA-N 0.000 description 2
- 241000972773 Aulopiformes Species 0.000 description 2
- 241000894006 Bacteria Species 0.000 description 2
- 241000282421 Canidae Species 0.000 description 2
- 108090000994 Catalytic RNA Proteins 0.000 description 2
- 102000053642 Catalytic RNA Human genes 0.000 description 2
- 108091026890 Coding region Proteins 0.000 description 2
- 108020004705 Codon Proteins 0.000 description 2
- KDXKERNSBIXSRK-RXMQYKEDSA-N D-lysine Chemical compound NCCCC[C@@H](N)C(O)=O KDXKERNSBIXSRK-RXMQYKEDSA-N 0.000 description 2
- 208000004986 Diffuse Cerebral Sclerosis of Schilder Diseases 0.000 description 2
- KCXVZYZYPLLWCC-UHFFFAOYSA-N EDTA Chemical compound OC(=O)CN(CC(O)=O)CCN(CC(O)=O)CC(O)=O KCXVZYZYPLLWCC-UHFFFAOYSA-N 0.000 description 2
- 241000196324 Embryophyta Species 0.000 description 2
- 101000941893 Felis catus Leucine-rich repeat and calponin homology domain-containing protein 1 Proteins 0.000 description 2
- 241000233866 Fungi Species 0.000 description 2
- WQZGKKKJIJFFOK-GASJEMHNSA-N Glucose Natural products OC[C@H]1OC(O)[C@H](O)[C@@H](O)[C@@H]1O WQZGKKKJIJFFOK-GASJEMHNSA-N 0.000 description 2
- PEDCQBHIVMGVHV-UHFFFAOYSA-N Glycerine Chemical compound OCC(O)CO PEDCQBHIVMGVHV-UHFFFAOYSA-N 0.000 description 2
- 239000004471 Glycine Substances 0.000 description 2
- 102100032563 Golgin subfamily A member 1 Human genes 0.000 description 2
- NYHBQMYGNKIUIF-UUOKFMHZSA-N Guanosine Chemical compound C1=NC=2C(=O)NC(N)=NC=2N1[C@@H]1O[C@H](CO)[C@@H](O)[C@H]1O NYHBQMYGNKIUIF-UUOKFMHZSA-N 0.000 description 2
- 101710088172 HTH-type transcriptional regulator RipA Proteins 0.000 description 2
- WZUVPPKBWHMQCE-UHFFFAOYSA-N Haematoxylin Chemical compound C12=CC(O)=C(O)C=C2CC2(O)C1C1=CC=C(O)C(O)=C1OC2 WZUVPPKBWHMQCE-UHFFFAOYSA-N 0.000 description 2
- 101000693765 Homo sapiens ATP-dependent 6-phosphofructokinase, platelet type Proteins 0.000 description 2
- 101000697529 Homo sapiens Stathmin-4 Proteins 0.000 description 2
- 101000788548 Homo sapiens Tubulin alpha-4A chain Proteins 0.000 description 2
- MHAJPDPJQMAIIY-UHFFFAOYSA-N Hydrogen peroxide Chemical compound OO MHAJPDPJQMAIIY-UHFFFAOYSA-N 0.000 description 2
- 108091092195 Intron Proteins 0.000 description 2
- 208000027747 Kennedy disease Diseases 0.000 description 2
- 241000124008 Mammalia Species 0.000 description 2
- 102100030412 Matrix metalloproteinase-9 Human genes 0.000 description 2
- 108700011259 MicroRNAs Proteins 0.000 description 2
- 108010025020 Nerve Growth Factor Proteins 0.000 description 2
- 102000007072 Nerve Growth Factors Human genes 0.000 description 2
- 208000028389 Nerve injury Diseases 0.000 description 2
- 208000012902 Nervous system disease Diseases 0.000 description 2
- 208000025966 Neurological disease Diseases 0.000 description 2
- 102000014736 Notch Human genes 0.000 description 2
- 108010070047 Notch Receptors Proteins 0.000 description 2
- 108091093105 Nuclear DNA Proteins 0.000 description 2
- 241000283973 Oryctolagus cuniculus Species 0.000 description 2
- 229910019142 PO4 Inorganic materials 0.000 description 2
- KPKZJLCSROULON-QKGLWVMZSA-N Phalloidin Chemical compound N1C(=O)[C@@H]([C@@H](O)C)NC(=O)[C@H](C)NC(=O)[C@H](C[C@@](C)(O)CO)NC(=O)[C@H](C2)NC(=O)[C@H](C)NC(=O)[C@@H]3C[C@H](O)CN3C(=O)[C@@H]1CSC1=C2C2=CC=CC=C2N1 KPKZJLCSROULON-QKGLWVMZSA-N 0.000 description 2
- 206010059440 Platelet toxicity Diseases 0.000 description 2
- 239000004698 Polyethylene Substances 0.000 description 2
- 239000002202 Polyethylene glycol Substances 0.000 description 2
- 102100024184 Polymerase delta-interacting protein 3 Human genes 0.000 description 2
- 102000004257 Potassium Channel Human genes 0.000 description 2
- 101710105008 RNA-binding protein Proteins 0.000 description 2
- 238000010240 RT-PCR analysis Methods 0.000 description 2
- FTALBRSUTCGOEG-UHFFFAOYSA-N Riluzole Chemical compound C1=C(OC(F)(F)F)C=C2SC(N)=NC2=C1 FTALBRSUTCGOEG-UHFFFAOYSA-N 0.000 description 2
- 108091027967 Small hairpin RNA Proteins 0.000 description 2
- DBMJMQXJHONAFJ-UHFFFAOYSA-M Sodium laurylsulphate Chemical compound [Na+].CCCCCCCCCCCCOS([O-])(=O)=O DBMJMQXJHONAFJ-UHFFFAOYSA-M 0.000 description 2
- 102100021796 Sonic hedgehog protein Human genes 0.000 description 2
- CZMRCDWAGMRECN-UGDNZRGBSA-N Sucrose Chemical compound O[C@H]1[C@H](O)[C@@H](CO)O[C@@]1(CO)O[C@@H]1[C@H](O)[C@@H](O)[C@H](O)[C@@H](CO)O1 CZMRCDWAGMRECN-UGDNZRGBSA-N 0.000 description 2
- NINIDFKCEFEMDL-UHFFFAOYSA-N Sulfur Chemical group [S] NINIDFKCEFEMDL-UHFFFAOYSA-N 0.000 description 2
- 102000008221 Superoxide Dismutase-1 Human genes 0.000 description 2
- 108010021188 Superoxide Dismutase-1 Proteins 0.000 description 2
- DHXVGJBLRPWPCS-UHFFFAOYSA-N Tetrahydropyran Chemical compound C1CCOCC1 DHXVGJBLRPWPCS-UHFFFAOYSA-N 0.000 description 2
- 102100025239 Tubulin alpha-4A chain Human genes 0.000 description 2
- ISAKRJDGNUQOIC-UHFFFAOYSA-N Uracil Chemical compound O=C1C=CNC(=O)N1 ISAKRJDGNUQOIC-UHFFFAOYSA-N 0.000 description 2
- DRTQHJPVMGBUCF-XVFCMESISA-N Uridine Chemical compound O[C@@H]1[C@H](O)[C@@H](CO)O[C@H]1N1C(=O)NC(=O)C=C1 DRTQHJPVMGBUCF-XVFCMESISA-N 0.000 description 2
- 208000006269 X-Linked Bulbo-Spinal Atrophy Diseases 0.000 description 2
- 238000002679 ablation Methods 0.000 description 2
- ZSLZBFCDCINBPY-ZSJPKINUSA-N acetyl-CoA Chemical compound O[C@@H]1[C@H](OP(O)(O)=O)[C@@H](COP(O)(=O)OP(O)(=O)OCC(C)(C)[C@@H](O)C(=O)NCCC(=O)NCCSC(=O)C)O[C@H]1N1C2=NC=NC(N)=C2N=C1 ZSLZBFCDCINBPY-ZSJPKINUSA-N 0.000 description 2
- 230000004913 activation Effects 0.000 description 2
- OIRDTQYFTABQOQ-KQYNXXCUSA-N adenosine Chemical compound C1=NC=2C(N)=NC=NC=2N1[C@@H]1O[C@H](CO)[C@@H](O)[C@H]1O OIRDTQYFTABQOQ-KQYNXXCUSA-N 0.000 description 2
- 238000004115 adherent culture Methods 0.000 description 2
- 239000008272 agar Substances 0.000 description 2
- 125000000217 alkyl group Chemical group 0.000 description 2
- 125000000304 alkynyl group Chemical group 0.000 description 2
- 229960000723 ampicillin Drugs 0.000 description 2
- 201000008257 amyotrophic lateral sclerosis type 1 Diseases 0.000 description 2
- 210000004102 animal cell Anatomy 0.000 description 2
- 230000010455 autoregulation Effects 0.000 description 2
- 230000008335 axon cargo transport Effects 0.000 description 2
- 230000003542 behavioural effect Effects 0.000 description 2
- 230000008901 benefit Effects 0.000 description 2
- WQZGKKKJIJFFOK-VFUOTHLCSA-N beta-D-glucose Chemical compound OC[C@H]1O[C@@H](O)[C@H](O)[C@@H](O)[C@@H]1O WQZGKKKJIJFFOK-VFUOTHLCSA-N 0.000 description 2
- 239000012620 biological material Substances 0.000 description 2
- 210000001124 body fluid Anatomy 0.000 description 2
- 239000010839 body fluid Substances 0.000 description 2
- 210000004899 c-terminal region Anatomy 0.000 description 2
- 125000004432 carbon atom Chemical group C* 0.000 description 2
- 238000004113 cell culture Methods 0.000 description 2
- 239000002458 cell surface marker Substances 0.000 description 2
- 230000005754 cellular signaling Effects 0.000 description 2
- 238000012512 characterization method Methods 0.000 description 2
- 239000003153 chemical reaction reagent Substances 0.000 description 2
- 238000012790 confirmation Methods 0.000 description 2
- 238000013270 controlled release Methods 0.000 description 2
- 238000004132 cross linking Methods 0.000 description 2
- 230000003436 cytoskeletal effect Effects 0.000 description 2
- 230000007812 deficiency Effects 0.000 description 2
- 238000013461 design Methods 0.000 description 2
- 239000003599 detergent Substances 0.000 description 2
- 230000009274 differential gene expression Effects 0.000 description 2
- 230000005782 double-strand break Effects 0.000 description 2
- 230000009977 dual effect Effects 0.000 description 2
- MMXKVMNBHPAILY-UHFFFAOYSA-N ethyl laurate Chemical compound CCCCCCCCCCCC(=O)OCC MMXKVMNBHPAILY-UHFFFAOYSA-N 0.000 description 2
- 230000002964 excitative effect Effects 0.000 description 2
- 230000001747 exhibiting effect Effects 0.000 description 2
- 238000002073 fluorescence micrograph Methods 0.000 description 2
- 150000002243 furanoses Chemical group 0.000 description 2
- 239000008103 glucose Substances 0.000 description 2
- 210000002288 golgi apparatus Anatomy 0.000 description 2
- 239000003102 growth factor Substances 0.000 description 2
- 125000001475 halogen functional group Chemical group 0.000 description 2
- 125000005843 halogen group Chemical group 0.000 description 2
- 230000000971 hippocampal effect Effects 0.000 description 2
- FDGQSTZJBFJUBT-UHFFFAOYSA-N hypoxanthine Chemical compound O=C1NC=NC2=C1NC=N2 FDGQSTZJBFJUBT-UHFFFAOYSA-N 0.000 description 2
- 238000002991 immunohistochemical analysis Methods 0.000 description 2
- 230000001939 inductive effect Effects 0.000 description 2
- 238000003780 insertion Methods 0.000 description 2
- 230000037431 insertion Effects 0.000 description 2
- 230000003993 interaction Effects 0.000 description 2
- 238000007918 intramuscular administration Methods 0.000 description 2
- 238000001990 intravenous administration Methods 0.000 description 2
- 238000002955 isolation Methods 0.000 description 2
- 125000005647 linker group Chemical group 0.000 description 2
- 239000007788 liquid Substances 0.000 description 2
- 229910001629 magnesium chloride Inorganic materials 0.000 description 2
- HQKMJHAJHXVSDF-UHFFFAOYSA-L magnesium stearate Chemical compound [Mg+2].CCCCCCCCCCCCCCCCCC([O-])=O.CCCCCCCCCCCCCCCCCC([O-])=O HQKMJHAJHXVSDF-UHFFFAOYSA-L 0.000 description 2
- 239000003550 marker Substances 0.000 description 2
- 239000000463 material Substances 0.000 description 2
- 108010082117 matrigel Proteins 0.000 description 2
- 238000001000 micrograph Methods 0.000 description 2
- 230000008880 microtubule cytoskeleton organization Effects 0.000 description 2
- 230000003278 mimic effect Effects 0.000 description 2
- 230000000394 mitotic effect Effects 0.000 description 2
- 230000009456 molecular mechanism Effects 0.000 description 2
- 238000012544 monitoring process Methods 0.000 description 2
- 238000010172 mouse model Methods 0.000 description 2
- 238000007837 multiplex assay Methods 0.000 description 2
- 210000003205 muscle Anatomy 0.000 description 2
- 230000036438 mutation frequency Effects 0.000 description 2
- 239000013642 negative control Substances 0.000 description 2
- 230000008764 nerve damage Effects 0.000 description 2
- 210000001178 neural stem cell Anatomy 0.000 description 2
- 210000000715 neuromuscular junction Anatomy 0.000 description 2
- 229910052757 nitrogen Inorganic materials 0.000 description 2
- 230000006780 non-homologous end joining Effects 0.000 description 2
- 238000010606 normalization Methods 0.000 description 2
- 230000030147 nuclear export Effects 0.000 description 2
- 238000012758 nuclear staining Methods 0.000 description 2
- 230000030648 nucleus localization Effects 0.000 description 2
- 229920001542 oligosaccharide Polymers 0.000 description 2
- 150000002482 oligosaccharides Chemical class 0.000 description 2
- 230000002018 overexpression Effects 0.000 description 2
- 125000004430 oxygen atom Chemical group O* 0.000 description 2
- 230000026792 palmitoylation Effects 0.000 description 2
- 239000008188 pellet Substances 0.000 description 2
- 235000021317 phosphate Nutrition 0.000 description 2
- 125000002467 phosphate group Chemical group [H]OP(=O)(O[H])O[*] 0.000 description 2
- 231100000201 platelet toxicity Toxicity 0.000 description 2
- 229920001223 polyethylene glycol Polymers 0.000 description 2
- 229920001282 polysaccharide Polymers 0.000 description 2
- 239000005017 polysaccharide Substances 0.000 description 2
- 150000004804 polysaccharides Chemical class 0.000 description 2
- 230000004481 post-translational protein modification Effects 0.000 description 2
- 230000001242 postsynaptic effect Effects 0.000 description 2
- 108020001213 potassium channel Proteins 0.000 description 2
- 230000003518 presynaptic effect Effects 0.000 description 2
- 230000000750 progressive effect Effects 0.000 description 2
- 230000001737 promoting effect Effects 0.000 description 2
- 239000003531 protein hydrolysate Substances 0.000 description 2
- 150000003212 purines Chemical class 0.000 description 2
- 150000003230 pyrimidines Chemical group 0.000 description 2
- 238000010814 radioimmunoprecipitation assay Methods 0.000 description 2
- 108020003175 receptors Proteins 0.000 description 2
- 230000001172 regenerating effect Effects 0.000 description 2
- 230000022532 regulation of transcription, DNA-dependent Effects 0.000 description 2
- 230000010410 reperfusion Effects 0.000 description 2
- 230000003252 repetitive effect Effects 0.000 description 2
- 238000010839 reverse transcription Methods 0.000 description 2
- 238000012552 review Methods 0.000 description 2
- 108091092562 ribozyme Proteins 0.000 description 2
- 229960004181 riluzole Drugs 0.000 description 2
- 235000019204 saccharin Nutrition 0.000 description 2
- CVHZOJJKTDOEJC-UHFFFAOYSA-N saccharin Chemical compound C1=CC=C2C(=O)NS(=O)(=O)C2=C1 CVHZOJJKTDOEJC-UHFFFAOYSA-N 0.000 description 2
- 229940081974 saccharin Drugs 0.000 description 2
- 239000000901 saccharin and its Na,K and Ca salt Substances 0.000 description 2
- 235000019515 salmon Nutrition 0.000 description 2
- 238000007480 sanger sequencing Methods 0.000 description 2
- 230000035945 sensitivity Effects 0.000 description 2
- 239000004055 small Interfering RNA Substances 0.000 description 2
- 150000003385 sodium Chemical class 0.000 description 2
- 235000019333 sodium laurylsulphate Nutrition 0.000 description 2
- 239000007787 solid Substances 0.000 description 2
- 208000002320 spinal muscular atrophy Diseases 0.000 description 2
- 230000037423 splicing regulation Effects 0.000 description 2
- 208000019929 sporadic amyotrophic lateral sclerosis Diseases 0.000 description 2
- UCSJYZPVAKXKNQ-HZYVHMACSA-N streptomycin Chemical compound CN[C@H]1[C@H](O)[C@@H](O)[C@H](CO)O[C@H]1O[C@@H]1[C@](C=O)(O)[C@H](C)O[C@H]1O[C@@H]1[C@@H](NC(N)=N)[C@H](O)[C@@H](NC(N)=N)[C@H](O)[C@H]1O UCSJYZPVAKXKNQ-HZYVHMACSA-N 0.000 description 2
- 230000004960 subcellular localization Effects 0.000 description 2
- 238000007920 subcutaneous administration Methods 0.000 description 2
- 238000006467 substitution reaction Methods 0.000 description 2
- 150000008163 sugars Chemical class 0.000 description 2
- 239000000725 suspension Substances 0.000 description 2
- 230000009885 systemic effect Effects 0.000 description 2
- 239000000454 talc Substances 0.000 description 2
- 229910052623 talc Inorganic materials 0.000 description 2
- 230000000699 topical effect Effects 0.000 description 2
- 231100000419 toxicity Toxicity 0.000 description 2
- 230000001988 toxicity Effects 0.000 description 2
- 230000005030 transcription termination Effects 0.000 description 2
- 230000014616 translation Effects 0.000 description 2
- 238000011311 validation assay Methods 0.000 description 2
- LNAZSHAWQACDHT-XIYTZBAFSA-N (2r,3r,4s,5r,6s)-4,5-dimethoxy-2-(methoxymethyl)-3-[(2s,3r,4s,5r,6r)-3,4,5-trimethoxy-6-(methoxymethyl)oxan-2-yl]oxy-6-[(2r,3r,4s,5r,6r)-4,5,6-trimethoxy-2-(methoxymethyl)oxan-3-yl]oxyoxane Chemical compound CO[C@@H]1[C@@H](OC)[C@H](OC)[C@@H](COC)O[C@H]1O[C@H]1[C@H](OC)[C@@H](OC)[C@H](O[C@H]2[C@@H]([C@@H](OC)[C@H](OC)O[C@@H]2COC)OC)O[C@@H]1COC LNAZSHAWQACDHT-XIYTZBAFSA-N 0.000 description 1
- 125000004169 (C1-C6) alkyl group Chemical group 0.000 description 1
- 101150084750 1 gene Proteins 0.000 description 1
- FYADHXFMURLYQI-UHFFFAOYSA-N 1,2,4-triazine Chemical group C1=CN=NC=N1 FYADHXFMURLYQI-UHFFFAOYSA-N 0.000 description 1
- DIIIISSCIXVANO-UHFFFAOYSA-N 1,2-Dimethylhydrazine Chemical compound CNNC DIIIISSCIXVANO-UHFFFAOYSA-N 0.000 description 1
- UHDGCWIWMRVCDJ-UHFFFAOYSA-N 1-beta-D-Xylofuranosyl-NH-Cytosine Natural products O=C1N=C(N)C=CN1C1C(O)C(O)C(CO)O1 UHDGCWIWMRVCDJ-UHFFFAOYSA-N 0.000 description 1
- MQLACMBJVPINKE-UHFFFAOYSA-N 10-[(3-hydroxy-4-methoxyphenyl)methylidene]anthracen-9-one Chemical compound C1=C(O)C(OC)=CC=C1C=C1C2=CC=CC=C2C(=O)C2=CC=CC=C21 MQLACMBJVPINKE-UHFFFAOYSA-N 0.000 description 1
- 108700020469 14-3-3 Proteins 0.000 description 1
- 102000004899 14-3-3 Proteins Human genes 0.000 description 1
- UHUHBFMZVCOEOV-UHFFFAOYSA-N 1h-imidazo[4,5-c]pyridin-4-amine Chemical compound NC1=NC=CC2=C1N=CN2 UHUHBFMZVCOEOV-UHFFFAOYSA-N 0.000 description 1
- QSHACTSJHMKXTE-UHFFFAOYSA-N 2-(2-aminopropyl)-7h-purin-6-amine Chemical compound CC(N)CC1=NC(N)=C2NC=NC2=N1 QSHACTSJHMKXTE-UHFFFAOYSA-N 0.000 description 1
- JRYMOPZHXMVHTA-DAGMQNCNSA-N 2-amino-7-[(2r,3r,4s,5r)-3,4-dihydroxy-5-(hydroxymethyl)oxolan-2-yl]-1h-pyrrolo[2,3-d]pyrimidin-4-one Chemical compound C1=CC=2C(=O)NC(N)=NC=2N1[C@@H]1O[C@H](CO)[C@@H](O)[C@H]1O JRYMOPZHXMVHTA-DAGMQNCNSA-N 0.000 description 1
- WKMPTBDYDNUJLF-UHFFFAOYSA-N 2-fluoroadenine Chemical compound NC1=NC(F)=NC2=C1N=CN2 WKMPTBDYDNUJLF-UHFFFAOYSA-N 0.000 description 1
- CFIBTBBTJWHPQV-UHFFFAOYSA-N 2-methyl-n-(6-oxo-3,7-dihydropurin-2-yl)propanamide Chemical compound N1C(NC(=O)C(C)C)=NC(=O)C2=C1N=CN2 CFIBTBBTJWHPQV-UHFFFAOYSA-N 0.000 description 1
- USCCECGPGBGFOM-UHFFFAOYSA-N 2-propyl-7h-purin-6-amine Chemical compound CCCC1=NC(N)=C2NC=NC2=N1 USCCECGPGBGFOM-UHFFFAOYSA-N 0.000 description 1
- CDOVNWNANFFLFJ-UHFFFAOYSA-N 4-[6-[4-(1-piperazinyl)phenyl]-3-pyrazolo[1,5-a]pyrimidinyl]quinoline Chemical compound C1CNCCN1C1=CC=C(C2=CN3N=CC(=C3N=C2)C=2C3=CC=CC=C3N=CC=2)C=C1 CDOVNWNANFFLFJ-UHFFFAOYSA-N 0.000 description 1
- FWMNVWWHGCHHJJ-SKKKGAJSSA-N 4-amino-1-[(2r)-6-amino-2-[[(2r)-2-[[(2r)-2-[[(2r)-2-amino-3-phenylpropanoyl]amino]-3-phenylpropanoyl]amino]-4-methylpentanoyl]amino]hexanoyl]piperidine-4-carboxylic acid Chemical compound C([C@H](C(=O)N[C@H](CC(C)C)C(=O)N[C@H](CCCCN)C(=O)N1CCC(N)(CC1)C(O)=O)NC(=O)[C@H](N)CC=1C=CC=CC=1)C1=CC=CC=C1 FWMNVWWHGCHHJJ-SKKKGAJSSA-N 0.000 description 1
- SIBMIRVJDKGAIZ-CWUIGSMPSA-N 5-(2-aminopropyl)-1-[(2r,3r,4s,5r)-3,4-dihydroxy-5-(hydroxymethyl)oxolan-2-yl]pyrimidine-2,4-dione Chemical compound O=C1NC(=O)C(CC(N)C)=CN1[C@H]1[C@H](O)[C@H](O)[C@@H](CO)O1 SIBMIRVJDKGAIZ-CWUIGSMPSA-N 0.000 description 1
- PTJWIQPHWPFNBW-MVIOUDGNSA-N 5-Ribosyluracil Natural products O=C1C([C@@H]2[C@@H](O)[C@H](O)[C@@H](CO)O2)=CNC(=O)N1 PTJWIQPHWPFNBW-MVIOUDGNSA-N 0.000 description 1
- KAXATBJARNMHAN-UHFFFAOYSA-N 5-benzoyl-1h-pyrimidine-2,4-dione Chemical compound C=1NC(=O)NC(=O)C=1C(=O)C1=CC=CC=C1 KAXATBJARNMHAN-UHFFFAOYSA-N 0.000 description 1
- AGFIRQJZCNVMCW-UAKXSSHOSA-N 5-bromouridine Chemical compound O[C@@H]1[C@H](O)[C@@H](CO)O[C@H]1N1C(=O)NC(=O)C(Br)=C1 AGFIRQJZCNVMCW-UAKXSSHOSA-N 0.000 description 1
- ZLAQATDNGLKIEV-UHFFFAOYSA-N 5-methyl-2-sulfanylidene-1h-pyrimidin-4-one Chemical compound CC1=CNC(=S)NC1=O ZLAQATDNGLKIEV-UHFFFAOYSA-N 0.000 description 1
- QQJXZVKXNSFHRI-UHFFFAOYSA-N 6-Benzamidopurine Chemical compound N=1C=NC=2N=CNC=2C=1NC(=O)C1=CC=CC=C1 QQJXZVKXNSFHRI-UHFFFAOYSA-N 0.000 description 1
- KXBCLNRMQPRVTP-UHFFFAOYSA-N 6-amino-1,5-dihydroimidazo[4,5-c]pyridin-4-one Chemical compound O=C1NC(N)=CC2=C1N=CN2 KXBCLNRMQPRVTP-UHFFFAOYSA-N 0.000 description 1
- DCPSTSVLRXOYGS-UHFFFAOYSA-N 6-amino-1h-pyrimidine-2-thione Chemical compound NC1=CC=NC(S)=N1 DCPSTSVLRXOYGS-UHFFFAOYSA-N 0.000 description 1
- QNNARSZPGNJZIX-UHFFFAOYSA-N 6-amino-5-prop-1-ynyl-1h-pyrimidin-2-one Chemical compound CC#CC1=CNC(=O)N=C1N QNNARSZPGNJZIX-UHFFFAOYSA-N 0.000 description 1
- CKOMXBHMKXXTNW-UHFFFAOYSA-N 6-methyladenine Chemical compound CNC1=NC=NC2=C1N=CN2 CKOMXBHMKXXTNW-UHFFFAOYSA-N 0.000 description 1
- LOSIULRWFAEMFL-UHFFFAOYSA-N 7-deazaguanine Chemical compound O=C1NC(N)=NC2=C1CC=N2 LOSIULRWFAEMFL-UHFFFAOYSA-N 0.000 description 1
- HBAQYPYDRFILMT-UHFFFAOYSA-N 8-[3-(1-cyclopropylpyrazol-4-yl)-1H-pyrazolo[4,3-d]pyrimidin-5-yl]-3-methyl-3,8-diazabicyclo[3.2.1]octan-2-one Chemical class C1(CC1)N1N=CC(=C1)C1=NNC2=C1N=C(N=C2)N1C2C(N(CC1CC2)C)=O HBAQYPYDRFILMT-UHFFFAOYSA-N 0.000 description 1
- HDZZVAMISRMYHH-UHFFFAOYSA-N 9beta-Ribofuranosyl-7-deazaadenin Natural products C1=CC=2C(N)=NC=NC=2N1C1OC(CO)C(O)C1O HDZZVAMISRMYHH-UHFFFAOYSA-N 0.000 description 1
- 101710163391 ADP-ribosyl cyclase/cyclic ADP-ribose hydrolase Proteins 0.000 description 1
- 101150102163 ATG7 gene Proteins 0.000 description 1
- 241000251468 Actinopterygii Species 0.000 description 1
- 108010085238 Actins Proteins 0.000 description 1
- 102000007469 Actins Human genes 0.000 description 1
- 208000011403 Alexander disease Diseases 0.000 description 1
- 208000023434 Alpers-Huttenlocher syndrome Diseases 0.000 description 1
- GUBGYTABKSRVRQ-XLOQQCSPSA-N Alpha-Lactose Chemical compound O[C@@H]1[C@@H](O)[C@@H](O)[C@@H](CO)O[C@H]1O[C@@H]1[C@@H](CO)O[C@H](O)[C@H](O)[C@H]1O GUBGYTABKSRVRQ-XLOQQCSPSA-N 0.000 description 1
- 102100028118 Annexin A11 Human genes 0.000 description 1
- 206010002961 Aplasia Diseases 0.000 description 1
- 102100022278 Arachidonate 5-lipoxygenase-activating protein Human genes 0.000 description 1
- DCXYFEDJOCDNAF-UHFFFAOYSA-N Asparagine Natural products OC(=O)C(N)CC(N)=O DCXYFEDJOCDNAF-UHFFFAOYSA-N 0.000 description 1
- 241000416162 Astragalus gummifer Species 0.000 description 1
- 206010003591 Ataxia Diseases 0.000 description 1
- 206010003594 Ataxia telangiectasia Diseases 0.000 description 1
- 102000007371 Ataxin-3 Human genes 0.000 description 1
- 102000014461 Ataxins Human genes 0.000 description 1
- 108010078286 Ataxins Proteins 0.000 description 1
- 241000282672 Ateles sp. Species 0.000 description 1
- 102000016613 Autophagy-Related Protein 7 Human genes 0.000 description 1
- 108010092778 Autophagy-Related Protein 7 Proteins 0.000 description 1
- 241000271566 Aves Species 0.000 description 1
- 241000157302 Bison bison athabascae Species 0.000 description 1
- 241000283690 Bos taurus Species 0.000 description 1
- 102100028252 Brain acid soluble protein 1 Human genes 0.000 description 1
- 206010052346 Brain contusion Diseases 0.000 description 1
- 206010048962 Brain oedema Diseases 0.000 description 1
- 206010068597 Bulbospinal muscular atrophy congenital Diseases 0.000 description 1
- 239000002126 C01EB10 - Adenosine Substances 0.000 description 1
- 238000010453 CRISPR/Cas method Methods 0.000 description 1
- OYPRJOBELJOOCE-UHFFFAOYSA-N Calcium Chemical compound [Ca] OYPRJOBELJOOCE-UHFFFAOYSA-N 0.000 description 1
- UXVMQQNJUSDDNG-UHFFFAOYSA-L Calcium chloride Chemical compound [Cl-].[Cl-].[Ca+2] UXVMQQNJUSDDNG-UHFFFAOYSA-L 0.000 description 1
- 208000022526 Canavan disease Diseases 0.000 description 1
- 241000282465 Canis Species 0.000 description 1
- 241000282472 Canis lupus familiaris Species 0.000 description 1
- OKTJSMMVPCPJKN-UHFFFAOYSA-N Carbon Chemical compound [C] OKTJSMMVPCPJKN-UHFFFAOYSA-N 0.000 description 1
- 229920002134 Carboxymethyl cellulose Polymers 0.000 description 1
- 206010008025 Cerebellar ataxia Diseases 0.000 description 1
- 241000282994 Cervidae Species 0.000 description 1
- 102100024297 Cilia- and flagella-associated protein 410 Human genes 0.000 description 1
- 208000018652 Closed Head injury Diseases 0.000 description 1
- 208000010200 Cockayne syndrome Diseases 0.000 description 1
- 102100023677 Coiled-coil-helix-coiled-coil-helix domain-containing protein 10, mitochondrial Human genes 0.000 description 1
- RYGMFSIKBFXOCR-UHFFFAOYSA-N Copper Chemical compound [Cu] RYGMFSIKBFXOCR-UHFFFAOYSA-N 0.000 description 1
- 229920002261 Corn starch Polymers 0.000 description 1
- 208000020406 Creutzfeldt Jacob disease Diseases 0.000 description 1
- 208000003407 Creutzfeldt-Jakob Syndrome Diseases 0.000 description 1
- 208000010859 Creutzfeldt-Jakob disease Diseases 0.000 description 1
- MIKUYHXYGGJMLM-GIMIYPNGSA-N Crotonoside Natural products C1=NC2=C(N)NC(=O)N=C2N1[C@H]1O[C@@H](CO)[C@H](O)[C@@H]1O MIKUYHXYGGJMLM-GIMIYPNGSA-N 0.000 description 1
- 102100038254 Cyclin-F Human genes 0.000 description 1
- UHDGCWIWMRVCDJ-PSQAKQOGSA-N Cytidine Natural products O=C1N=C(N)C=CN1[C@@H]1[C@@H](O)[C@@H](O)[C@H](CO)O1 UHDGCWIWMRVCDJ-PSQAKQOGSA-N 0.000 description 1
- 102000010831 Cytoskeletal Proteins Human genes 0.000 description 1
- 108010037414 Cytoskeletal Proteins Proteins 0.000 description 1
- 102100032620 Cytotoxic granule associated RNA binding protein TIA1 Human genes 0.000 description 1
- FBPFZTCFMRRESA-FSIIMWSLSA-N D-Glucitol Natural products OC[C@H](O)[C@H](O)[C@@H](O)[C@H](O)CO FBPFZTCFMRRESA-FSIIMWSLSA-N 0.000 description 1
- FBPFZTCFMRRESA-KVTDHHQDSA-N D-Mannitol Chemical compound OC[C@@H](O)[C@@H](O)[C@H](O)[C@H](O)CO FBPFZTCFMRRESA-KVTDHHQDSA-N 0.000 description 1
- FBPFZTCFMRRESA-JGWLITMVSA-N D-glucitol Chemical compound OC[C@H](O)[C@@H](O)[C@H](O)[C@H](O)CO FBPFZTCFMRRESA-JGWLITMVSA-N 0.000 description 1
- RGHNJXZEOKUKBD-SQOUGZDYSA-M D-gluconate Chemical compound OC[C@@H](O)[C@@H](O)[C@H](O)[C@@H](O)C([O-])=O RGHNJXZEOKUKBD-SQOUGZDYSA-M 0.000 description 1
- NYHBQMYGNKIUIF-UHFFFAOYSA-N D-guanosine Natural products C1=2NC(N)=NC(=O)C=2N=CN1C1OC(CO)C(O)C1O NYHBQMYGNKIUIF-UHFFFAOYSA-N 0.000 description 1
- DWJXYEABWRJFSP-XOBRGWDASA-N DAPT Chemical compound N([C@@H](C)C(=O)N[C@H](C(=O)OC(C)(C)C)C=1C=CC=CC=1)C(=O)CC1=CC(F)=CC(F)=C1 DWJXYEABWRJFSP-XOBRGWDASA-N 0.000 description 1
- 102000004163 DNA-directed RNA polymerases Human genes 0.000 description 1
- 108090000626 DNA-directed RNA polymerases Proteins 0.000 description 1
- 206010012289 Dementia Diseases 0.000 description 1
- 206010067889 Dementia with Lewy bodies Diseases 0.000 description 1
- 208000000202 Diffuse Axonal Injury Diseases 0.000 description 1
- 206010061818 Disease progression Diseases 0.000 description 1
- 201000010374 Down Syndrome Diseases 0.000 description 1
- 241000271559 Dromaiidae Species 0.000 description 1
- 206010013887 Dysarthria Diseases 0.000 description 1
- LVGKNOAMLMIIKO-UHFFFAOYSA-N Elaidinsaeure-aethylester Natural products CCCCCCCCC=CCCCCCCCC(=O)OCC LVGKNOAMLMIIKO-UHFFFAOYSA-N 0.000 description 1
- 206010049020 Encephalitis periaxialis diffusa Diseases 0.000 description 1
- 102000004190 Enzymes Human genes 0.000 description 1
- 108090000790 Enzymes Proteins 0.000 description 1
- 102100030751 Eomesodermin homolog Human genes 0.000 description 1
- 241000283086 Equidae Species 0.000 description 1
- 241000283074 Equus asinus Species 0.000 description 1
- 108700039887 Essential Genes Proteins 0.000 description 1
- 239000001856 Ethyl cellulose Substances 0.000 description 1
- ZZSNKZQZMQGXPY-UHFFFAOYSA-N Ethyl cellulose Chemical compound CCOCC1OC(OC)C(OCC)C(OCC)C1OC1C(O)C(O)C(OC)C(CO)O1 ZZSNKZQZMQGXPY-UHFFFAOYSA-N 0.000 description 1
- 108010077781 F-actin-binding proteins Proteins 0.000 description 1
- 229940124602 FDA-approved drug Drugs 0.000 description 1
- 241000282324 Felis Species 0.000 description 1
- 241000282326 Felis catus Species 0.000 description 1
- 240000008168 Ficus benjamina Species 0.000 description 1
- 238000012413 Fluorescence activated cell sorting analysis Methods 0.000 description 1
- 208000024412 Friedreich ataxia Diseases 0.000 description 1
- 241000287828 Gallus gallus Species 0.000 description 1
- 101000935687 Gallus gallus Brain acid soluble protein 1 homolog Proteins 0.000 description 1
- 108010010803 Gelatin Proteins 0.000 description 1
- 208000010055 Globoid Cell Leukodystrophy Diseases 0.000 description 1
- 230000025545 Golgi localization Effects 0.000 description 1
- 102100021181 Golgi phosphoprotein 3 Human genes 0.000 description 1
- 208000035895 Guillain-Barré syndrome Diseases 0.000 description 1
- 206010019196 Head injury Diseases 0.000 description 1
- 101000768066 Homo sapiens Annexin A11 Proteins 0.000 description 1
- 101000755875 Homo sapiens Arachidonate 5-lipoxygenase-activating protein Proteins 0.000 description 1
- 101000935689 Homo sapiens Brain acid soluble protein 1 Proteins 0.000 description 1
- 101000980066 Homo sapiens Cilia- and flagella-associated protein 410 Proteins 0.000 description 1
- 101000907013 Homo sapiens Coiled-coil-helix-coiled-coil-helix domain-containing protein 10, mitochondrial Proteins 0.000 description 1
- 101000884183 Homo sapiens Cyclin-F Proteins 0.000 description 1
- 101000654853 Homo sapiens Cytotoxic granule associated RNA binding protein TIA1 Proteins 0.000 description 1
- 101001064167 Homo sapiens Eomesodermin homolog Proteins 0.000 description 1
- 101001040734 Homo sapiens Golgi phosphoprotein 3 Proteins 0.000 description 1
- 101000693844 Homo sapiens Insulin-like growth factor-binding protein complex acid labile subunit Proteins 0.000 description 1
- 101001139062 Homo sapiens Kinesin heavy chain isoform 5A Proteins 0.000 description 1
- 101000957559 Homo sapiens Matrin-3 Proteins 0.000 description 1
- 101000990902 Homo sapiens Matrix metalloproteinase-9 Proteins 0.000 description 1
- 101000950695 Homo sapiens Mitogen-activated protein kinase 8 Proteins 0.000 description 1
- 101000979249 Homo sapiens Neuromodulin Proteins 0.000 description 1
- 101000873418 Homo sapiens P-selectin glycoprotein ligand 1 Proteins 0.000 description 1
- 101000579123 Homo sapiens Phosphoglycerate kinase 1 Proteins 0.000 description 1
- 101000575639 Homo sapiens Ribonucleoside-diphosphate reductase subunit M2 Proteins 0.000 description 1
- 101100422584 Homo sapiens STMN2 gene Proteins 0.000 description 1
- 101001123846 Homo sapiens Serine/threonine-protein kinase Nek1 Proteins 0.000 description 1
- 101000868139 Homo sapiens Sortilin Proteins 0.000 description 1
- 101000595526 Homo sapiens T-box brain protein 1 Proteins 0.000 description 1
- 108010001336 Horseradish Peroxidase Proteins 0.000 description 1
- 238000009015 Human TaqMan MicroRNA Assay kit Methods 0.000 description 1
- 241000713772 Human immunodeficiency virus 1 Species 0.000 description 1
- 208000023105 Huntington disease Diseases 0.000 description 1
- 206010020751 Hypersensitivity Diseases 0.000 description 1
- UGQMRVRMYYASKQ-UHFFFAOYSA-N Hypoxanthine nucleoside Natural products OC1C(O)C(CO)OC1N1C(NC=NC2=O)=C2N=C1 UGQMRVRMYYASKQ-UHFFFAOYSA-N 0.000 description 1
- DGAQECJNVWCQMB-PUAWFVPOSA-M Ilexoside XXIX Chemical compound C[C@@H]1CC[C@@]2(CC[C@@]3(C(=CC[C@H]4[C@]3(CC[C@@H]5[C@@]4(CC[C@@H](C5(C)C)OS(=O)(=O)[O-])C)C)[C@@H]2[C@]1(C)O)C)C(=O)O[C@H]6[C@@H]([C@H]([C@@H]([C@H](O6)CO)O)O)O.[Na+] DGAQECJNVWCQMB-PUAWFVPOSA-M 0.000 description 1
- 208000032382 Ischaemic stroke Diseases 0.000 description 1
- 101150070110 Isl1 gene Proteins 0.000 description 1
- 102100020685 Kinesin heavy chain isoform 5A Human genes 0.000 description 1
- 208000028226 Krabbe disease Diseases 0.000 description 1
- ONIBWKKTOPOVIA-BYPYZUCNSA-N L-Proline Chemical compound OC(=O)[C@@H]1CCCN1 ONIBWKKTOPOVIA-BYPYZUCNSA-N 0.000 description 1
- DCXYFEDJOCDNAF-REOHCLBHSA-N L-asparagine Chemical compound OC(=O)[C@@H](N)CC(N)=O DCXYFEDJOCDNAF-REOHCLBHSA-N 0.000 description 1
- GUBGYTABKSRVRQ-QKKXKWKRSA-N Lactose Natural products OC[C@H]1O[C@@H](O[C@H]2[C@H](O)[C@@H](O)C(O)O[C@@H]2CO)[C@H](O)[C@@H](O)[C@H]1O GUBGYTABKSRVRQ-QKKXKWKRSA-N 0.000 description 1
- 201000002832 Lewy body dementia Diseases 0.000 description 1
- 102000003960 Ligases Human genes 0.000 description 1
- 108090000364 Ligases Proteins 0.000 description 1
- 108060001084 Luciferase Proteins 0.000 description 1
- 239000005089 Luciferase Substances 0.000 description 1
- KDXKERNSBIXSRK-UHFFFAOYSA-N Lysine Natural products NCCCCC(N)C(O)=O KDXKERNSBIXSRK-UHFFFAOYSA-N 0.000 description 1
- 239000004472 Lysine Substances 0.000 description 1
- 108091077621 MAPRE family Proteins 0.000 description 1
- 241000282553 Macaca Species 0.000 description 1
- 241000282567 Macaca fascicularis Species 0.000 description 1
- 241000282560 Macaca mulatta Species 0.000 description 1
- 208000002569 Machado-Joseph Disease Diseases 0.000 description 1
- FYYHWMGAXLPEAU-UHFFFAOYSA-N Magnesium Chemical compound [Mg] FYYHWMGAXLPEAU-UHFFFAOYSA-N 0.000 description 1
- 229930195725 Mannitol Natural products 0.000 description 1
- 102100038645 Matrin-3 Human genes 0.000 description 1
- 108010015302 Matrix metalloproteinase-9 Proteins 0.000 description 1
- 208000036626 Mental retardation Diseases 0.000 description 1
- 229920000168 Microcrystalline cellulose Polymers 0.000 description 1
- 206010049567 Miller Fisher syndrome Diseases 0.000 description 1
- 102100037808 Mitogen-activated protein kinase 8 Human genes 0.000 description 1
- 208000001089 Multiple system atrophy Diseases 0.000 description 1
- 241001529936 Murinae Species 0.000 description 1
- 208000008238 Muscle Spasticity Diseases 0.000 description 1
- 108010021466 Mutant Proteins Proteins 0.000 description 1
- 102000008300 Mutant Proteins Human genes 0.000 description 1
- 201000002481 Myositis Diseases 0.000 description 1
- 206010068871 Myotonic dystrophy Diseases 0.000 description 1
- VQAYFKKCNSOZKM-IOSLPCCCSA-N N(6)-methyladenosine Chemical compound C1=NC=2C(NC)=NC=NC=2N1[C@@H]1O[C@H](CO)[C@@H](O)[C@H]1O VQAYFKKCNSOZKM-IOSLPCCCSA-N 0.000 description 1
- GXCLVBGFBYZDAG-UHFFFAOYSA-N N-[2-(1H-indol-3-yl)ethyl]-N-methylprop-2-en-1-amine Chemical compound CN(CCC1=CNC2=C1C=CC=C2)CC=C GXCLVBGFBYZDAG-UHFFFAOYSA-N 0.000 description 1
- VQAYFKKCNSOZKM-UHFFFAOYSA-N NSC 29409 Natural products C1=NC=2C(NC)=NC=NC=2N1C1OC(CO)C(O)C1O VQAYFKKCNSOZKM-UHFFFAOYSA-N 0.000 description 1
- 206010028980 Neoplasm Diseases 0.000 description 1
- 102100023206 Neuromodulin Human genes 0.000 description 1
- 208000002537 Neuronal Ceroid-Lipofuscinoses Diseases 0.000 description 1
- 102100031801 Nexilin Human genes 0.000 description 1
- 108091092724 Noncoding DNA Proteins 0.000 description 1
- 108010077850 Nuclear Localization Signals Proteins 0.000 description 1
- 102100034925 P-selectin glycoprotein ligand 1 Human genes 0.000 description 1
- 238000002944 PCR assay Methods 0.000 description 1
- KJWZYMMLVHIVSU-IYCNHOCDSA-N PGK1 Chemical compound CCCCC[C@H](O)\C=C\[C@@H]1[C@@H](CCCCCCC(O)=O)C(=O)CC1=O KJWZYMMLVHIVSU-IYCNHOCDSA-N 0.000 description 1
- 241000282579 Pan Species 0.000 description 1
- 206010033799 Paralysis Diseases 0.000 description 1
- 235000019483 Peanut oil Nutrition 0.000 description 1
- 208000028361 Penetrating Head injury Diseases 0.000 description 1
- 108010009711 Phalloidine Proteins 0.000 description 1
- 102100028251 Phosphoglycerate kinase 1 Human genes 0.000 description 1
- 102000007982 Phosphoproteins Human genes 0.000 description 1
- 108010089430 Phosphoproteins Proteins 0.000 description 1
- 208000000609 Pick Disease of the Brain Diseases 0.000 description 1
- 101710142722 Polymerase delta-interacting protein 3 Proteins 0.000 description 1
- ZLMJMSJWJFRBEC-UHFFFAOYSA-N Potassium Chemical compound [K] ZLMJMSJWJFRBEC-UHFFFAOYSA-N 0.000 description 1
- 206010036631 Presenile dementia Diseases 0.000 description 1
- 208000032319 Primary lateral sclerosis Diseases 0.000 description 1
- 102000019204 Progranulins Human genes 0.000 description 1
- 108010012809 Progranulins Proteins 0.000 description 1
- ONIBWKKTOPOVIA-UHFFFAOYSA-N Proline Natural products OC(=O)C1CCCN1 ONIBWKKTOPOVIA-UHFFFAOYSA-N 0.000 description 1
- KDCGOANMDULRCW-UHFFFAOYSA-N Purine Natural products N1=CNC2=NC=NC2=C1 KDCGOANMDULRCW-UHFFFAOYSA-N 0.000 description 1
- CZPWVGJYEJSRLH-UHFFFAOYSA-N Pyrimidine Chemical compound C1=CN=CN=C1 CZPWVGJYEJSRLH-UHFFFAOYSA-N 0.000 description 1
- 108020003584 RNA Isoforms Proteins 0.000 description 1
- 238000002123 RNA extraction Methods 0.000 description 1
- 239000013614 RNA sample Substances 0.000 description 1
- 108700020471 RNA-Binding Proteins Proteins 0.000 description 1
- 230000004570 RNA-binding Effects 0.000 description 1
- 238000011530 RNeasy Mini Kit Methods 0.000 description 1
- 208000005587 Refsum Disease Diseases 0.000 description 1
- 102100026006 Ribonucleoside-diphosphate reductase subunit M2 Human genes 0.000 description 1
- 235000019485 Safflower oil Nutrition 0.000 description 1
- 241000277331 Salmonidae Species 0.000 description 1
- 208000021811 Sandhoff disease Diseases 0.000 description 1
- 208000021235 Schilder disease Diseases 0.000 description 1
- 108091081021 Sense strand Proteins 0.000 description 1
- 102100028751 Serine/threonine-protein kinase Nek1 Human genes 0.000 description 1
- 102000007562 Serum Albumin Human genes 0.000 description 1
- 108010071390 Serum Albumin Proteins 0.000 description 1
- 208000021386 Sjogren Syndrome Diseases 0.000 description 1
- 208000009415 Spinocerebellar Ataxias Diseases 0.000 description 1
- 208000036834 Spinocerebellar ataxia type 3 Diseases 0.000 description 1
- 201000003629 Spinocerebellar ataxia type 8 Diseases 0.000 description 1
- 229920002472 Starch Polymers 0.000 description 1
- 108050007361 Stathmin-4 Proteins 0.000 description 1
- 241000271567 Struthioniformes Species 0.000 description 1
- 229930006000 Sucrose Natural products 0.000 description 1
- 241000282887 Suidae Species 0.000 description 1
- 102100036083 T-box brain protein 1 Human genes 0.000 description 1
- RYYWUUFWQRZTIU-UHFFFAOYSA-N Thiophosphoric acid Chemical class OP(O)(S)=O RYYWUUFWQRZTIU-UHFFFAOYSA-N 0.000 description 1
- 229920001615 Tragacanth Polymers 0.000 description 1
- 239000007983 Tris buffer Substances 0.000 description 1
- 229920004890 Triton X-100 Polymers 0.000 description 1
- 239000013504 Triton X-100 Substances 0.000 description 1
- 108090000848 Ubiquitin Proteins 0.000 description 1
- 102000044159 Ubiquitin Human genes 0.000 description 1
- 206010046298 Upper motor neurone lesion Diseases 0.000 description 1
- 240000008042 Zea mays Species 0.000 description 1
- 235000005824 Zea mays ssp. parviglumis Nutrition 0.000 description 1
- 235000002017 Zea mays subsp mays Nutrition 0.000 description 1
- 238000010521 absorption reaction Methods 0.000 description 1
- 230000001133 acceleration Effects 0.000 description 1
- 108010076089 accutase Proteins 0.000 description 1
- 229940100228 acetyl coenzyme a Drugs 0.000 description 1
- 239000013543 active substance Substances 0.000 description 1
- 230000001154 acute effect Effects 0.000 description 1
- 125000002015 acyclic group Chemical group 0.000 description 1
- 230000008649 adaptation response Effects 0.000 description 1
- 101150063416 add gene Proteins 0.000 description 1
- 229960005305 adenosine Drugs 0.000 description 1
- 208000030597 adult Refsum disease Diseases 0.000 description 1
- 239000000443 aerosol Substances 0.000 description 1
- 239000011543 agarose gel Substances 0.000 description 1
- 239000000783 alginic acid Substances 0.000 description 1
- 235000010443 alginic acid Nutrition 0.000 description 1
- 229920000615 alginic acid Polymers 0.000 description 1
- 229960001126 alginic acid Drugs 0.000 description 1
- 150000004781 alginic acids Chemical class 0.000 description 1
- 125000003342 alkenyl group Chemical group 0.000 description 1
- WNROFYMDJYEPJX-UHFFFAOYSA-K aluminium hydroxide Chemical compound [OH-].[OH-].[OH-].[Al+3] WNROFYMDJYEPJX-UHFFFAOYSA-K 0.000 description 1
- AVKUERGKIZMTKX-NJBDSQKTSA-N ampicillin Chemical compound C1([C@@H](N)C(=O)N[C@H]2[C@H]3SC([C@@H](N3C2=O)C(O)=O)(C)C)=CC=CC=C1 AVKUERGKIZMTKX-NJBDSQKTSA-N 0.000 description 1
- 230000003321 amplification Effects 0.000 description 1
- 238000000137 annealing Methods 0.000 description 1
- 239000000427 antigen Substances 0.000 description 1
- 108091007433 antigens Proteins 0.000 description 1
- 102000036639 antigens Human genes 0.000 description 1
- 239000003963 antioxidant agent Substances 0.000 description 1
- 238000003491 array Methods 0.000 description 1
- 229960001230 asparagine Drugs 0.000 description 1
- 235000009582 asparagine Nutrition 0.000 description 1
- 210000001130 astrocyte Anatomy 0.000 description 1
- 201000004562 autosomal dominant cerebellar ataxia Diseases 0.000 description 1
- 208000021018 autosomal dominant inheritance Diseases 0.000 description 1
- 208000013404 behavioral symptom Diseases 0.000 description 1
- 230000009286 beneficial effect Effects 0.000 description 1
- DRTQHJPVMGBUCF-PSQAKQOGSA-N beta-L-uridine Natural products O[C@H]1[C@@H](O)[C@H](CO)O[C@@H]1N1C(=O)NC(=O)C=C1 DRTQHJPVMGBUCF-PSQAKQOGSA-N 0.000 description 1
- 230000008436 biogenesis Effects 0.000 description 1
- 229920001222 biopolymer Polymers 0.000 description 1
- 230000001851 biosynthetic effect Effects 0.000 description 1
- 210000004369 blood Anatomy 0.000 description 1
- 239000008280 blood Substances 0.000 description 1
- 239000005388 borosilicate glass Substances 0.000 description 1
- 229960001467 bortezomib Drugs 0.000 description 1
- GXJABQQUPOEUTA-RDJZCZTQSA-N bortezomib Chemical compound C([C@@H](C(=O)N[C@@H](CC(C)C)B(O)O)NC(=O)C=1N=CC=NC=1)C1=CC=CC=C1 GXJABQQUPOEUTA-RDJZCZTQSA-N 0.000 description 1
- 230000009516 brain contusion Effects 0.000 description 1
- 208000006752 brain edema Diseases 0.000 description 1
- 239000004067 bulking agent Substances 0.000 description 1
- 239000011575 calcium Substances 0.000 description 1
- 229910052791 calcium Inorganic materials 0.000 description 1
- 239000001110 calcium chloride Substances 0.000 description 1
- 229910001628 calcium chloride Inorganic materials 0.000 description 1
- 235000011148 calcium chloride Nutrition 0.000 description 1
- 201000011510 cancer Diseases 0.000 description 1
- 239000002775 capsule Substances 0.000 description 1
- 239000001768 carboxy methyl cellulose Substances 0.000 description 1
- 235000010948 carboxy methyl cellulose Nutrition 0.000 description 1
- 239000008112 carboxymethyl-cellulose Substances 0.000 description 1
- 241001233037 catfish Species 0.000 description 1
- 230000030833 cell death Effects 0.000 description 1
- 230000024245 cell differentiation Effects 0.000 description 1
- 239000006285 cell suspension Substances 0.000 description 1
- 230000003833 cell viability Effects 0.000 description 1
- 230000035289 cell-matrix adhesion Effects 0.000 description 1
- 210000003570 cell-matrix junction Anatomy 0.000 description 1
- 230000007248 cellular mechanism Effects 0.000 description 1
- 239000001913 cellulose Substances 0.000 description 1
- 229920002678 cellulose Polymers 0.000 description 1
- 235000010980 cellulose Nutrition 0.000 description 1
- 229920002301 cellulose acetate Polymers 0.000 description 1
- 238000007385 chemical modification Methods 0.000 description 1
- 235000013330 chicken meat Nutrition 0.000 description 1
- 230000001684 chronic effect Effects 0.000 description 1
- 239000007979 citrate buffer Substances 0.000 description 1
- 238000003776 cleavage reaction Methods 0.000 description 1
- 239000011248 coating agent Substances 0.000 description 1
- 229940110456 cocoa butter Drugs 0.000 description 1
- 235000019868 cocoa butter Nutrition 0.000 description 1
- 230000007278 cognition impairment Effects 0.000 description 1
- 230000001149 cognitive effect Effects 0.000 description 1
- 239000003086 colorant Substances 0.000 description 1
- 238000010835 comparative analysis Methods 0.000 description 1
- 239000003184 complementary RNA Substances 0.000 description 1
- 230000009918 complex formation Effects 0.000 description 1
- 230000001010 compromised effect Effects 0.000 description 1
- 239000003636 conditioned culture medium Substances 0.000 description 1
- 230000001276 controlling effect Effects 0.000 description 1
- 229910052802 copper Inorganic materials 0.000 description 1
- 239000010949 copper Substances 0.000 description 1
- 235000005822 corn Nutrition 0.000 description 1
- 235000005687 corn oil Nutrition 0.000 description 1
- 239000002285 corn oil Substances 0.000 description 1
- 238000012937 correction Methods 0.000 description 1
- 230000002596 correlated effect Effects 0.000 description 1
- 230000001054 cortical effect Effects 0.000 description 1
- 210000003618 cortical neuron Anatomy 0.000 description 1
- 235000012343 cottonseed oil Nutrition 0.000 description 1
- 239000002385 cottonseed oil Substances 0.000 description 1
- 239000006071 cream Substances 0.000 description 1
- 210000004748 cultured cell Anatomy 0.000 description 1
- 238000012258 culturing Methods 0.000 description 1
- UHDGCWIWMRVCDJ-ZAKLUEHWSA-N cytidine Chemical compound O=C1N=C(N)C=CN1[C@H]1[C@H](O)[C@@H](O)[C@H](CO)O1 UHDGCWIWMRVCDJ-ZAKLUEHWSA-N 0.000 description 1
- 238000004163 cytometry Methods 0.000 description 1
- 210000000805 cytoplasm Anatomy 0.000 description 1
- 210000004292 cytoskeleton Anatomy 0.000 description 1
- 210000000172 cytosol Anatomy 0.000 description 1
- 231100000135 cytotoxicity Toxicity 0.000 description 1
- 230000003013 cytotoxicity Effects 0.000 description 1
- 230000034994 death Effects 0.000 description 1
- 230000003412 degenerative effect Effects 0.000 description 1
- 210000001787 dendrite Anatomy 0.000 description 1
- 230000002638 denervation Effects 0.000 description 1
- 229960003964 deoxycholic acid Drugs 0.000 description 1
- KXGVEGMKQFWNSR-LLQZFEROSA-N deoxycholic acid Chemical compound C([C@H]1CC2)[C@H](O)CC[C@]1(C)[C@@H]1[C@@H]2[C@@H]2CC[C@H]([C@@H](CCC(O)=O)C)[C@@]2(C)[C@@H](O)C1 KXGVEGMKQFWNSR-LLQZFEROSA-N 0.000 description 1
- 230000000368 destabilizing effect Effects 0.000 description 1
- 230000001627 detrimental effect Effects 0.000 description 1
- 230000009521 diffuse axonal injury Effects 0.000 description 1
- 230000029087 digestion Effects 0.000 description 1
- 230000005750 disease progression Effects 0.000 description 1
- KPUWHANPEXNPJT-UHFFFAOYSA-N disiloxane Chemical class [SiH3]O[SiH3] KPUWHANPEXNPJT-UHFFFAOYSA-N 0.000 description 1
- 239000006185 dispersion Substances 0.000 description 1
- 238000002224 dissection Methods 0.000 description 1
- 238000010494 dissociation reaction Methods 0.000 description 1
- 230000005593 dissociations Effects 0.000 description 1
- NAGJZTKCGNOGPW-UHFFFAOYSA-N dithiophosphoric acid Chemical class OP(O)(S)=S NAGJZTKCGNOGPW-UHFFFAOYSA-N 0.000 description 1
- 239000002552 dosage form Substances 0.000 description 1
- 231100000673 dose–response relationship Toxicity 0.000 description 1
- 239000008298 dragée Substances 0.000 description 1
- 238000012377 drug delivery Methods 0.000 description 1
- 238000007877 drug screening Methods 0.000 description 1
- 238000011977 dual antiplatelet therapy Methods 0.000 description 1
- 230000004064 dysfunction Effects 0.000 description 1
- 230000008482 dysregulation Effects 0.000 description 1
- 230000008143 early embryonic development Effects 0.000 description 1
- QELUYTUMUWHWMC-UHFFFAOYSA-N edaravone Chemical compound O=C1CC(C)=NN1C1=CC=CC=C1 QELUYTUMUWHWMC-UHFFFAOYSA-N 0.000 description 1
- 229950009041 edaravone Drugs 0.000 description 1
- 238000001962 electrophoresis Methods 0.000 description 1
- 230000013020 embryo development Effects 0.000 description 1
- 210000001671 embryonic stem cell Anatomy 0.000 description 1
- 210000002257 embryonic structure Anatomy 0.000 description 1
- 230000002996 emotional effect Effects 0.000 description 1
- 239000003797 essential amino acid Substances 0.000 description 1
- 235000020776 essential amino acid Nutrition 0.000 description 1
- 150000002148 esters Chemical class 0.000 description 1
- 235000019325 ethyl cellulose Nutrition 0.000 description 1
- 229920001249 ethyl cellulose Polymers 0.000 description 1
- LVGKNOAMLMIIKO-QXMHVHEDSA-N ethyl oleate Chemical compound CCCCCCCC\C=C/CCCCCCCC(=O)OCC LVGKNOAMLMIIKO-QXMHVHEDSA-N 0.000 description 1
- 229940093471 ethyl oleate Drugs 0.000 description 1
- 230000000763 evoking effect Effects 0.000 description 1
- 210000002950 fibroblast Anatomy 0.000 description 1
- 239000000945 filler Substances 0.000 description 1
- 238000010304 firing Methods 0.000 description 1
- 239000000796 flavoring agent Substances 0.000 description 1
- 235000013355 food flavoring agent Nutrition 0.000 description 1
- 230000037406 food intake Effects 0.000 description 1
- 235000003599 food sweetener Nutrition 0.000 description 1
- 210000000609 ganglia Anatomy 0.000 description 1
- 238000003304 gavage Methods 0.000 description 1
- 238000001502 gel electrophoresis Methods 0.000 description 1
- 239000008273 gelatin Substances 0.000 description 1
- 229920000159 gelatin Polymers 0.000 description 1
- 235000019322 gelatine Nutrition 0.000 description 1
- 235000011852 gelatine desserts Nutrition 0.000 description 1
- 238000012252 genetic analysis Methods 0.000 description 1
- 238000012908 genetic validation Methods 0.000 description 1
- 239000011521 glass Substances 0.000 description 1
- 230000002518 glial effect Effects 0.000 description 1
- 229940050410 gluconate Drugs 0.000 description 1
- 230000000848 glutamatergic effect Effects 0.000 description 1
- ZDXPYRJPNDTMRX-UHFFFAOYSA-N glutamine Natural products OC(=O)C(N)CCC(N)=O ZDXPYRJPNDTMRX-UHFFFAOYSA-N 0.000 description 1
- 235000011187 glycerol Nutrition 0.000 description 1
- 125000003630 glycyl group Chemical group [H]N([H])C([H])([H])C(*)=O 0.000 description 1
- 229940029575 guanosine Drugs 0.000 description 1
- 125000000623 heterocyclic group Chemical group 0.000 description 1
- 210000004295 hippocampal neuron Anatomy 0.000 description 1
- 238000007489 histopathology method Methods 0.000 description 1
- DLINORNFHVEIFE-UHFFFAOYSA-N hydrogen peroxide;zinc Chemical compound [Zn].OO DLINORNFHVEIFE-UHFFFAOYSA-N 0.000 description 1
- 230000002209 hydrophobic effect Effects 0.000 description 1
- 238000003384 imaging method Methods 0.000 description 1
- 238000011493 immune profiling Methods 0.000 description 1
- 230000002055 immunohistochemical effect Effects 0.000 description 1
- 238000003364 immunohistochemistry Methods 0.000 description 1
- 210000003000 inclusion body Anatomy 0.000 description 1
- 229910052738 indium Inorganic materials 0.000 description 1
- 239000004615 ingredient Substances 0.000 description 1
- 230000000977 initiatory effect Effects 0.000 description 1
- 230000000266 injurious effect Effects 0.000 description 1
- 238000001361 intraarterial administration Methods 0.000 description 1
- 230000003834 intracellular effect Effects 0.000 description 1
- 238000000185 intracerebroventricular administration Methods 0.000 description 1
- 238000007917 intracranial administration Methods 0.000 description 1
- 238000007912 intraperitoneal administration Methods 0.000 description 1
- 238000011835 investigation Methods 0.000 description 1
- 230000007794 irritation Effects 0.000 description 1
- 208000017476 juvenile neuronal ceroid lipofuscinosis Diseases 0.000 description 1
- 206010023497 kuru Diseases 0.000 description 1
- 238000002372 labelling Methods 0.000 description 1
- 239000008101 lactose Substances 0.000 description 1
- 201000010901 lateral sclerosis Diseases 0.000 description 1
- 239000004973 liquid crystal related substance Substances 0.000 description 1
- 230000007774 longterm Effects 0.000 description 1
- 239000007937 lozenge Substances 0.000 description 1
- 239000000314 lubricant Substances 0.000 description 1
- 238000004020 luminiscence type Methods 0.000 description 1
- 210000004072 lung Anatomy 0.000 description 1
- 239000006166 lysate Substances 0.000 description 1
- 239000011777 magnesium Substances 0.000 description 1
- 229910052749 magnesium Inorganic materials 0.000 description 1
- VTHJTEIRLNZDEV-UHFFFAOYSA-L magnesium dihydroxide Chemical compound [OH-].[OH-].[Mg+2] VTHJTEIRLNZDEV-UHFFFAOYSA-L 0.000 description 1
- 239000000347 magnesium hydroxide Substances 0.000 description 1
- 229910001862 magnesium hydroxide Inorganic materials 0.000 description 1
- 235000019359 magnesium stearate Nutrition 0.000 description 1
- 239000000594 mannitol Substances 0.000 description 1
- 235000010355 mannitol Nutrition 0.000 description 1
- 238000013507 mapping Methods 0.000 description 1
- 230000035800 maturation Effects 0.000 description 1
- 238000002483 medication Methods 0.000 description 1
- 210000002901 mesenchymal stem cell Anatomy 0.000 description 1
- 229960001252 methamphetamine Drugs 0.000 description 1
- MYWUZJCMWCOHBA-VIFPVBQESA-N methamphetamine Chemical compound CN[C@@H](C)CC1=CC=CC=C1 MYWUZJCMWCOHBA-VIFPVBQESA-N 0.000 description 1
- 229920000609 methyl cellulose Polymers 0.000 description 1
- 239000001923 methylcellulose Substances 0.000 description 1
- 235000010981 methylcellulose Nutrition 0.000 description 1
- 125000001570 methylene group Chemical group [H]C([H])([*:1])[*:2] 0.000 description 1
- YACKEPLHDIMKIO-UHFFFAOYSA-N methylphosphonic acid Chemical class CP(O)(O)=O YACKEPLHDIMKIO-UHFFFAOYSA-N 0.000 description 1
- 108091070501 miRNA Proteins 0.000 description 1
- 235000019813 microcrystalline cellulose Nutrition 0.000 description 1
- 239000008108 microcrystalline cellulose Substances 0.000 description 1
- 229940016286 microcrystalline cellulose Drugs 0.000 description 1
- 201000011540 mitochondrial DNA depletion syndrome 4a Diseases 0.000 description 1
- 230000004879 molecular function Effects 0.000 description 1
- 230000003990 molecular pathway Effects 0.000 description 1
- 238000013425 morphometry Methods 0.000 description 1
- 230000007659 motor function Effects 0.000 description 1
- 201000006417 multiple sclerosis Diseases 0.000 description 1
- 238000002887 multiple sequence alignment Methods 0.000 description 1
- 230000000869 mutational effect Effects 0.000 description 1
- XBDUZBHKKUFFRH-UHFFFAOYSA-N n-(2-oxo-1h-pyrimidin-6-yl)benzamide Chemical compound OC1=NC=CC(NC(=O)C=2C=CC=CC=2)=N1 XBDUZBHKKUFFRH-UHFFFAOYSA-N 0.000 description 1
- FMKLITBCOZWOEX-UHFFFAOYSA-N n-(5-methyl-2-oxo-1h-pyrimidin-6-yl)benzamide Chemical compound CC1=CNC(=O)N=C1NC(=O)C1=CC=CC=C1 FMKLITBCOZWOEX-UHFFFAOYSA-N 0.000 description 1
- 210000004897 n-terminal region Anatomy 0.000 description 1
- 230000032405 negative regulation of neuron apoptotic process Effects 0.000 description 1
- 229910052754 neon Inorganic materials 0.000 description 1
- GKAOGPIIYCISHV-UHFFFAOYSA-N neon atom Chemical compound [Ne] GKAOGPIIYCISHV-UHFFFAOYSA-N 0.000 description 1
- 230000007992 neural conversion Effects 0.000 description 1
- 210000005155 neural progenitor cell Anatomy 0.000 description 1
- 238000003522 neurite outgrowth assay Methods 0.000 description 1
- 230000007472 neurodevelopment Effects 0.000 description 1
- 230000004766 neurogenesis Effects 0.000 description 1
- 230000000926 neurological effect Effects 0.000 description 1
- 208000018360 neuromuscular disease Diseases 0.000 description 1
- 201000007607 neuronal ceroid lipofuscinosis 3 Diseases 0.000 description 1
- 230000006764 neuronal dysfunction Effects 0.000 description 1
- 230000007996 neuronal plasticity Effects 0.000 description 1
- 230000009689 neuronal regeneration Effects 0.000 description 1
- 230000006576 neuronal survival Effects 0.000 description 1
- 230000004723 neuronal vulnerability Effects 0.000 description 1
- 239000002858 neurotransmitter agent Substances 0.000 description 1
- 230000000508 neurotrophic effect Effects 0.000 description 1
- 239000003900 neurotrophic factor Substances 0.000 description 1
- 238000007481 next generation sequencing Methods 0.000 description 1
- 125000004433 nitrogen atom Chemical group N* 0.000 description 1
- 210000000929 nociceptor Anatomy 0.000 description 1
- 108091008700 nociceptors Proteins 0.000 description 1
- 231100000252 nontoxic Toxicity 0.000 description 1
- 230000003000 nontoxic effect Effects 0.000 description 1
- 238000003199 nucleic acid amplification method Methods 0.000 description 1
- 102000044158 nucleic acid binding protein Human genes 0.000 description 1
- 108700020942 nucleic acid binding protein Proteins 0.000 description 1
- QIQXTHQIDYTFRH-UHFFFAOYSA-N octadecanoic acid Chemical compound CCCCCCCCCCCCCCCCCC(O)=O QIQXTHQIDYTFRH-UHFFFAOYSA-N 0.000 description 1
- 229920002113 octoxynol Polymers 0.000 description 1
- 239000003921 oil Substances 0.000 description 1
- 235000019198 oils Nutrition 0.000 description 1
- 239000002674 ointment Substances 0.000 description 1
- 239000004006 olive oil Substances 0.000 description 1
- 235000008390 olive oil Nutrition 0.000 description 1
- 239000006174 pH buffer Substances 0.000 description 1
- 125000001312 palmitoyl group Chemical group O=C([*])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])C([H])([H])[H] 0.000 description 1
- 238000007911 parenteral administration Methods 0.000 description 1
- 230000003950 pathogenic mechanism Effects 0.000 description 1
- 239000000312 peanut oil Substances 0.000 description 1
- 239000002304 perfume Substances 0.000 description 1
- 230000002093 peripheral effect Effects 0.000 description 1
- 102000013415 peroxidase activity proteins Human genes 0.000 description 1
- 108040007629 peroxidase activity proteins Proteins 0.000 description 1
- 239000000575 pesticide Substances 0.000 description 1
- 230000000144 pharmacologic effect Effects 0.000 description 1
- 238000012247 phenotypical assay Methods 0.000 description 1
- NBIIXXVUZAFLBC-UHFFFAOYSA-K phosphate Chemical compound [O-]P([O-])([O-])=O NBIIXXVUZAFLBC-UHFFFAOYSA-K 0.000 description 1
- 239000010452 phosphate Substances 0.000 description 1
- 150000004713 phosphodiesters Chemical class 0.000 description 1
- 150000003013 phosphoric acid derivatives Chemical class 0.000 description 1
- 125000004437 phosphorous atom Chemical group 0.000 description 1
- LFGREXWGYUGZLY-UHFFFAOYSA-N phosphoryl Chemical group [P]=O LFGREXWGYUGZLY-UHFFFAOYSA-N 0.000 description 1
- 230000026731 phosphorylation Effects 0.000 description 1
- 238000006366 phosphorylation reaction Methods 0.000 description 1
- 230000000865 phosphorylative effect Effects 0.000 description 1
- 125000005642 phosphothioate group Chemical group 0.000 description 1
- 239000006187 pill Substances 0.000 description 1
- 229920000155 polyglutamine Polymers 0.000 description 1
- 108010040003 polyglutamine Proteins 0.000 description 1
- 229920005862 polyol Polymers 0.000 description 1
- 150000003077 polyols Chemical class 0.000 description 1
- 229920000136 polysorbate Polymers 0.000 description 1
- 239000013641 positive control Substances 0.000 description 1
- 230000020775 positive regulation of microtubule depolymerization Effects 0.000 description 1
- 230000029279 positive regulation of transcription, DNA-dependent Effects 0.000 description 1
- 239000011591 potassium Substances 0.000 description 1
- 229910052700 potassium Inorganic materials 0.000 description 1
- 229920001592 potato starch Polymers 0.000 description 1
- 230000003334 potential effect Effects 0.000 description 1
- 230000003389 potentiating effect Effects 0.000 description 1
- 239000000843 powder Substances 0.000 description 1
- 239000003755 preservative agent Substances 0.000 description 1
- 238000000513 principal component analysis Methods 0.000 description 1
- 230000008569 process Effects 0.000 description 1
- 201000002212 progressive supranuclear palsy Diseases 0.000 description 1
- 230000002062 proliferating effect Effects 0.000 description 1
- 230000000644 propagated effect Effects 0.000 description 1
- QQONPFPTGQHPMA-UHFFFAOYSA-N propylene Natural products CC=C QQONPFPTGQHPMA-UHFFFAOYSA-N 0.000 description 1
- 125000004805 propylene group Chemical group [H]C([H])([H])C([H])([*:1])C([H])([H])[*:2] 0.000 description 1
- 230000001681 protective effect Effects 0.000 description 1
- 230000006916 protein interaction Effects 0.000 description 1
- 230000009145 protein modification Effects 0.000 description 1
- 238000001243 protein synthesis Methods 0.000 description 1
- PTJWIQPHWPFNBW-GBNDHIKLSA-N pseudouridine Chemical compound O[C@@H]1[C@H](O)[C@@H](CO)O[C@H]1C1=CNC(=O)NC1=O PTJWIQPHWPFNBW-GBNDHIKLSA-N 0.000 description 1
- IGFXRKMLLMBKSA-UHFFFAOYSA-N purine Chemical compound N1=C[N]C2=NC=NC2=C1 IGFXRKMLLMBKSA-UHFFFAOYSA-N 0.000 description 1
- UBQKCCHYAOITMY-UHFFFAOYSA-N pyridin-2-ol Chemical compound OC1=CC=CC=N1 UBQKCCHYAOITMY-UHFFFAOYSA-N 0.000 description 1
- 238000004445 quantitative analysis Methods 0.000 description 1
- 210000000664 rectum Anatomy 0.000 description 1
- 230000014891 regulation of alternative nuclear mRNA splicing, via spliceosome Effects 0.000 description 1
- 230000023276 regulation of development, heterochronic Effects 0.000 description 1
- 230000029058 respiratory gaseous exchange Effects 0.000 description 1
- 210000002345 respiratory system Anatomy 0.000 description 1
- 210000004708 ribosome subunit Anatomy 0.000 description 1
- 235000005713 safflower oil Nutrition 0.000 description 1
- 239000003813 safflower oil Substances 0.000 description 1
- 230000007017 scission Effects 0.000 description 1
- 238000005204 segregation Methods 0.000 description 1
- 238000002864 sequence alignment Methods 0.000 description 1
- 239000008159 sesame oil Substances 0.000 description 1
- 235000011803 sesame oil Nutrition 0.000 description 1
- 230000003584 silencer Effects 0.000 description 1
- 239000002924 silencing RNA Substances 0.000 description 1
- 210000002027 skeletal muscle Anatomy 0.000 description 1
- 230000008410 smoothened signaling pathway Effects 0.000 description 1
- 239000011734 sodium Substances 0.000 description 1
- 229910052708 sodium Inorganic materials 0.000 description 1
- 235000015424 sodium Nutrition 0.000 description 1
- 239000011780 sodium chloride Substances 0.000 description 1
- 238000002415 sodium dodecyl sulfate polyacrylamide gel electrophoresis Methods 0.000 description 1
- 239000002904 solvent Substances 0.000 description 1
- 239000000600 sorbitol Substances 0.000 description 1
- 235000010356 sorbitol Nutrition 0.000 description 1
- 239000003549 soybean oil Substances 0.000 description 1
- 235000012424 soybean oil Nutrition 0.000 description 1
- 238000001228 spectrum Methods 0.000 description 1
- 208000020431 spinal cord injury Diseases 0.000 description 1
- 201000003594 spinocerebellar ataxia type 12 Diseases 0.000 description 1
- 239000007921 spray Substances 0.000 description 1
- 230000006641 stabilisation Effects 0.000 description 1
- 238000011105 stabilization Methods 0.000 description 1
- 235000019698 starch Nutrition 0.000 description 1
- 239000008174 sterile solution Substances 0.000 description 1
- 229960005322 streptomycin Drugs 0.000 description 1
- 239000005720 sucrose Substances 0.000 description 1
- CCEKAJIANROZEO-UHFFFAOYSA-N sulfluramid Chemical group CCNS(=O)(=O)C(F)(F)C(F)(F)C(F)(F)C(F)(F)C(F)(F)C(F)(F)C(F)(F)C(F)(F)F CCEKAJIANROZEO-UHFFFAOYSA-N 0.000 description 1
- 229910052717 sulfur Inorganic materials 0.000 description 1
- 239000011593 sulfur Substances 0.000 description 1
- 210000002222 superior cervical ganglion Anatomy 0.000 description 1
- 230000003319 supportive effect Effects 0.000 description 1
- 239000000829 suppository Substances 0.000 description 1
- 230000004083 survival effect Effects 0.000 description 1
- 230000009747 swallowing Effects 0.000 description 1
- 230000003976 synaptic dysfunction Effects 0.000 description 1
- 208000011580 syndromic disease Diseases 0.000 description 1
- 238000007910 systemic administration Methods 0.000 description 1
- 239000003826 tablet Substances 0.000 description 1
- 235000012222 talc Nutrition 0.000 description 1
- 229940124597 therapeutic agent Drugs 0.000 description 1
- RYYWUUFWQRZTIU-UHFFFAOYSA-K thiophosphate Chemical compound [O-]P([O-])([O-])=S RYYWUUFWQRZTIU-UHFFFAOYSA-K 0.000 description 1
- 231100000331 toxic Toxicity 0.000 description 1
- 230000002588 toxic effect Effects 0.000 description 1
- 239000000196 tragacanth Substances 0.000 description 1
- 235000010487 tragacanth Nutrition 0.000 description 1
- 229940116362 tragacanth Drugs 0.000 description 1
- 238000012546 transfer Methods 0.000 description 1
- 230000001052 transient effect Effects 0.000 description 1
- 238000013519 translation Methods 0.000 description 1
- LENZDBCJOHFCAS-UHFFFAOYSA-N tris Chemical compound OCC(N)(CO)CO LENZDBCJOHFCAS-UHFFFAOYSA-N 0.000 description 1
- HDZZVAMISRMYHH-KCGFPETGSA-N tubercidin Chemical compound C1=CC=2C(N)=NC=NC=2N1[C@@H]1O[C@H](CO)[C@@H](O)[C@H]1O HDZZVAMISRMYHH-KCGFPETGSA-N 0.000 description 1
- 238000011144 upstream manufacturing Methods 0.000 description 1
- 229940035893 uracil Drugs 0.000 description 1
- DRTQHJPVMGBUCF-UHFFFAOYSA-N uracil arabinoside Natural products OC1C(O)C(CO)OC1N1C(=O)NC(=O)C=C1 DRTQHJPVMGBUCF-UHFFFAOYSA-N 0.000 description 1
- 229940045145 uridine Drugs 0.000 description 1
- 239000003981 vehicle Substances 0.000 description 1
- 230000028973 vesicle-mediated transport Effects 0.000 description 1
- 230000001018 virulence Effects 0.000 description 1
- 238000005406 washing Methods 0.000 description 1
- 239000001993 wax Substances 0.000 description 1
- 239000000080 wetting agent Substances 0.000 description 1
- 229940075420 xanthine Drugs 0.000 description 1
- XOOUIPVCVHRTMJ-UHFFFAOYSA-L zinc stearate Chemical compound [Zn+2].CCCCCCCCCCCCCCCCCC([O-])=O.CCCCCCCCCCCCCCCCCC([O-])=O XOOUIPVCVHRTMJ-UHFFFAOYSA-L 0.000 description 1
Images
Classifications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/11—DNA or RNA fragments; Modified forms thereof; Non-coding nucleic acids having a biological activity
- C12N15/113—Non-coding nucleic acids modulating the expression of genes, e.g. antisense oligonucleotides; Antisense DNA or RNA; Triplex- forming oligonucleotides; Catalytic nucleic acids, e.g. ribozymes; Nucleic acids used in co-suppression or gene silencing
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61P—SPECIFIC THERAPEUTIC ACTIVITY OF CHEMICAL COMPOUNDS OR MEDICINAL PREPARATIONS
- A61P25/00—Drugs for disorders of the nervous system
- A61P25/28—Drugs for disorders of the nervous system for treating neurodegenerative disorders of the central nervous system, e.g. nootropic agents, cognition enhancers, drugs for treating Alzheimer's disease or other forms of dementia
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2310/00—Structure or type of the nucleic acid
- C12N2310/10—Type of nucleic acid
- C12N2310/11—Antisense
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2310/00—Structure or type of the nucleic acid
- C12N2310/30—Chemical structure
- C12N2310/31—Chemical structure of the backbone
- C12N2310/315—Phosphorothioates
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2310/00—Structure or type of the nucleic acid
- C12N2310/30—Chemical structure
- C12N2310/31—Chemical structure of the backbone
- C12N2310/316—Phosphonothioates
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2310/00—Structure or type of the nucleic acid
- C12N2310/30—Chemical structure
- C12N2310/32—Chemical structure of the sugar
- C12N2310/323—Chemical structure of the sugar modified ring structure
- C12N2310/3231—Chemical structure of the sugar modified ring structure having an additional ring, e.g. LNA, ENA
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N2320/00—Applications; Uses
- C12N2320/30—Special therapeutic applications
- C12N2320/33—Alteration of splicing
Landscapes
- Health & Medical Sciences (AREA)
- Engineering & Computer Science (AREA)
- Life Sciences & Earth Sciences (AREA)
- Biomedical Technology (AREA)
- Genetics & Genomics (AREA)
- Bioinformatics & Cheminformatics (AREA)
- Chemical & Material Sciences (AREA)
- Organic Chemistry (AREA)
- Biotechnology (AREA)
- General Engineering & Computer Science (AREA)
- Wood Science & Technology (AREA)
- Zoology (AREA)
- Molecular Biology (AREA)
- General Health & Medical Sciences (AREA)
- Neurology (AREA)
- Neurosurgery (AREA)
- Biochemistry (AREA)
- Physics & Mathematics (AREA)
- Plant Pathology (AREA)
- Microbiology (AREA)
- Biophysics (AREA)
- Medicinal Chemistry (AREA)
- Psychiatry (AREA)
- Chemical Kinetics & Catalysis (AREA)
- General Chemical & Material Sciences (AREA)
- Hospice & Palliative Care (AREA)
- Nuclear Medicine, Radiotherapy & Molecular Imaging (AREA)
- Pharmacology & Pharmacy (AREA)
- Animal Behavior & Ethology (AREA)
- Public Health (AREA)
- Veterinary Medicine (AREA)
- Pharmaceuticals Containing Other Organic And Inorganic Compounds (AREA)
- Medicines That Contain Protein Lipid Enzymes And Other Medicines (AREA)
- Measuring Or Testing Involving Enzymes Or Micro-Organisms (AREA)
Abstract
本開示は、対象の神経細胞におけるTDP病変またはTDP-43の機能性の減退に関連する疾患または状態を処置するための、及び不完全なまたは変化したSTMN2 RNA配列の包含を抑制または防止する候補薬剤を同定するための、組成物及び方法に関する。
Description
関連出願
本出願は、2021年1月4日に出願された米国仮特許出願第63/133,749号、2020年8月7日に出願された米国仮特許出願第63/063,174号、及び2020年3月25日に出願された米国仮特許出願第62/994,797号に対する優先権を主張する。上記出願の教示全体は、参照により本明細書に組み込まれる。
本出願は、2021年1月4日に出願された米国仮特許出願第63/133,749号、2020年8月7日に出願された米国仮特許出願第63/063,174号、及び2020年3月25日に出願された米国仮特許出願第62/994,797号に対する優先権を主張する。上記出願の教示全体は、参照により本明細書に組み込まれる。
筋萎縮性側索硬化症(ALS)は、上位運動ニューロン及び下位運動ニューロンの両方の選択的喪失を特徴とする致死性の神経変性疾患である(1)。ALS患者は進行性麻痺を経験し、発声困難、嚥下困難、及び最終的には呼吸困難を発症し(2、3)、通常、診断時から1~5年後にこの疾患により死亡する。疾患の進行を若干変化させる2つのFDA承認薬を除いて(4)、ALSの処置は支持療法に限られている。ALSは現在、初老期認知症の最も一般的な原因である前頭側頭型認知症(FTD)と同じ臨床的及び病理学的範囲にあると認識されている。FTDは、効果的な処置が存在しない、行動の変化、言語障害、及び実行機能の喪失を特徴とする(5)。ほとんどのALS及びFTD症例の病因は依然として不明であるが、病理学的所見及び家族ベースの連鎖研究により、両疾患に関与する分子経路に重複があることが実証されている(1、6)。
Klim JR,Williams LA,Limone F,Guerra San Juan I,Davis-Dusenbery BN,Mordes DA,Burberry A,Steinbaugh MJ,Gamage KK,Kirchner R,Moccia R,Cassel SH,Chen K,Wainger BJ,Woolf CJ,Eggan K.ALS-implicated protein TDP-43 sustains levels of STMN2,a mediator of motor neuron growth and repair.Nat Neurosci.2019;22(2):167-79.Epub 2019/01/16.doi:10.1038/s41593-018-0300-4.PubMed PMID:30643292.
Melamed Z,Lopez-Erauskin J,Baughn MW,Zhang O,Drenner K,Sun Y,Freyermuth F,McMahon MA,Beccari MS,Artates JW,Ohkubo T,Rodriguez M,Lin N,Wu D,Bennett CF,Rigo F,Da Cruz S,Ravits J,Lagier-Tourenne C,Cleveland DW.Premature polyadenylation-mediated loss of stathmin-2 is a hallmark of TDP-43-dependent neurodegeneration.Nat Neurosci.2019;22(2):180-90.Epub 2019/01/16.doi: 10.1038/s41593-018-0293-z.PubMed PMID:30643298;PMCID:PMC6348009.
Prudencio M,Humphrey J,Pickles S,Brown AL,Hill SE,Kachergus J,Shi J,Heckman M,Spiegel M,Cook C,Song Y,Yue M,Daughrity L,Carlomagno Y,Jansen-West K,Fernandez De Castro C,DeTure M,Koga S,Wang YC,Sivakumar P,Bodo C,Candalija A,Talbot K,Selvaraj BT,Burr K,Chandran S,Newcombe J,Lashley T,Hubbard I,Catalano D,Kim D,Propp N,Fennessey S,Fagegaltier D,Phatnani H,Secrier M,Fisher EM,Oskarsson B,van Blitterswijk M,Rademakers R,Graff-Radford NR,Boeve B,Knopman DS,Petersen R,Josephs K,Thompson EA,Raj T,Ward ME,Dickson D,Gendron TF,Fratta P,Petrucelli L.Truncated stathmin-2 is a marker of TDP-43 pathology in frontotemporal dementia.J Clin Invest.2020.Epub 2020/08/14.doi:10.1172/JCI139741.PubMed PMID:32790644.
van Eersel J,Ke YD,Gladbach A,Bi M,Gotz J,Kril JJ,Ittner LM.Cytoplasmic accumulation and aggregation of TDP-43 upon proteasome inhibition in cultured neurons.PLoS One.2011;6(7):e22850.Epub 2011/08/11.doi:10.1371/journal.pone.0022850.PubMed PMID:21829535;PMCID:PMC3146516.
Shin JE,Miller BR,Babetto E,Cho Y,Sasaki Y,Qayum S,Russler EV,Cavalli V,Milbrandt J,DiAntonio A.SCG10 is a JNK target in the axonal degeneration pathway.Proc Natl Acad Sci U S A.2012;109(52):E3696-705.Epub 2012/11/29.doi:10.1073/pnas.1216204109.PubMed PMID:23188802;PMCID:PMC3535671.
TDP-43は、主に核内DNA/RNA結合タンパク質であり、転写調節、スプライシング、プレマイクロRNAプロセシング、ストレス顆粒形成、ならびにメッセンジャーRNAの輸送及び安定性において機能的役割を有する。TDP-43は、ALS及びFTDの多くの散発性症例における封入体の主要構成成分であることが見出された。TDP-43の異常な発現に応答して、STMN2レベルの低下が見られる。SCG10としても知られるSTMN2は、微小管安定性の調節因子であり、正常ヒト運動ニューロンの成長及び修復に必要なタンパク質をコードすることが示されてきた。本明細書には、STMN2レベルを回復または増加させるための方法及び組成物が記載される。
本明細書には、STMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、それにより不完全なまたは変化したSTMN2 RNA配列の包含を抑制または防止するアンチセンスオリゴヌクレオチドが開示される。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、STMN2 RNA配列のポリアデニル化部位に結合しない。いくつかの実施形態では、不完全なまたは変化したSTMN2 RNA配列は、TDP-43の機能が減退しているかまたはTDP病変が存在する場合に発生しかつ存在量が増加する。
本明細書には、STMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、それにより不完全なまたは変化したSTMN2 RNA配列の包含を抑制または防止するアンチセンスオリゴヌクレオチドが開示される。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、STMN2 RNA配列のポリアデニル化部位に結合しない。いくつかの実施形態では、不完全なまたは変化したSTMN2 RNA配列は、TDP-43の機能が減退しているかまたはTDP病変が存在する場合に発生しかつ存在量が増加する。
本明細書では、潜在性エクソンをコードするSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、それによりSTMN2 RNAへの潜在性エクソンの包含を抑制または防止するアンチセンスオリゴヌクレオチドであって、STMN2 mRNA配列、プレmRNA配列、または新生RNA配列のポリアデニル化部位に結合しないアンチセンスオリゴヌクレオチドもまた開示される。
本明細書では、STMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、STMN2タンパク質発現を増加させるアンチセンスオリゴヌクレオチドが更に開示される。
いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、5’スプライス部位、3’スプライス部位、または通常のTDP-43結合部位を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、1つ以上のスプライス部位を標的とする。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とするように設計されている。
いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、血小板毒性を呈さない。
本明細書では、配列番号37~85からなる群から選択される配列を含むアンチセンスオリゴヌクレオチドもまた開示される。いくつかの態様では、アンチセンスオリゴヌクレオチドは、配列番号37~74からなる群から選択される配列を含む。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含むか、またはより具体的には、アンチセンスオリゴヌクレオチドは、配列番号52を含み得る。特定の実施形態では、アンチセンスオリゴヌクレオチドは、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含むか、またはより具体的には、アンチセンスオリゴヌクレオチドは、配列番号73または配列番号53を含む。
本明細書では、配列番号37~85からなる群から選択される配列を含む1つ以上のアンチセンスオリゴヌクレオチドを含む医薬組成物が更に開示される。いくつかの実施形態では、1つ以上のアンチセンスオリゴヌクレオチドは、配列番号37~74からなる群から選択される配列を含む。いくつかの実施形態では、1つ以上のアンチセンスオリゴヌクレオチドは、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含むか、またはより具体的には、1つ以上のアンチセンスオリゴヌクレオチドは、配列番号52を含み得る。特定の実施形態では、アンチセンスオリゴヌクレオチドは、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含むか、またはより具体的には、アンチセンスオリゴヌクレオチドは、配列番号73または配列番号53を含む。
本明細書では、多量体オリゴヌクレオチドを含む医薬組成物が開示される。多量体オリゴヌクレオチドは、配列番号37~85からなる群から選択される1つ以上の配列を含む。いくつかの実施形態では、多量体オリゴヌクレオチドは、配列番号37~85からなる群から選択される2つ以上の配列を含む。多量体オリゴヌクレオチドは、配列の複数のコピーを含んでもよく、または代わりに複数の配列の単一コピーを含んでもよい。
いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、STMN2 RNAへの潜在性エクソンの包含を抑制または防止する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、例えば、潜在性エクソンをコードするSTMN2 RNA配列、プレmRNA配列、または新生RNA配列に特異的に結合する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、STMN2タンパク質の分解を防止するかまたは遅延させる。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、STMN2タンパク質を増加させる。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、5’スプライス部位、3’スプライス部位、または通常のTDP-43結合部位を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、一本鎖領域、例えば、TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、潜在性スプライス部位の近位部位、早期ポリアデニル化部位の近位部位、または潜在性スプライス部位と早期ポリアデニル化部位との間に位置する部位を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、構造化されていない潜在性エクソン内の標的領域に結合する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、TDP-43により調節される5’スプライス部位の近傍にまたはそれに隣接して結合する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、予測されるTDP-43結合部位の近位領域を標的とする。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、TDP-43の通常の結合部位を標的とする。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、1つ以上のスプライス部位を標的とする。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、潜在性スプライシングを抑制する。
いくつかの実施形態では、医薬組成物は、2つ以上のアンチセンスオリゴヌクレオチドを含み、いくつかの態様では、3つ以上のアンチセンスオリゴヌクレオチドを含む。いくつかの実施形態では、2つ以上のアンチセンスオリゴヌクレオチドは、共有結合されている。いくつかの実施形態では、1つ以上のアンチセンスオリゴヌクレオチドは、STMN2タンパク質発現を増加させる。
いくつかの実施形態では、医薬組成物は、神経変性疾患を処置するための薬剤、外傷性脳損傷を処置するための薬剤、またはプロテアソーム阻害剤誘導性ニューロパチーを処置するための薬剤を更に含む。いくつかの実施形態では、医薬組成物は、遺伝子治療薬としてSTMN2を更に含む。いくつかの実施形態では、医薬組成物は、JNK阻害剤を更に含む。
本明細書では、TAR DNA結合タンパク質43(TDP-43)の機能性の減退に関連する疾患もしくは状態を処置すること、またはその疾患もしくは状態の可能性を低減させることを必要とする対象の神経細胞における、その疾患もしくは状態を処置するか、またはその疾患もしくは状態の可能性を低減させる方法もまた開示される。本方法は、STMN2タンパク質のレベルの低減を補正するアンチセンスオリゴヌクレオチドに神経細胞を接触させることを含み得、この薬剤は、標的転写物のポリアデニル化部位を標的としない。
本明細書では、TAR DNA結合タンパク質43(TDP-43)の機能性の減退に関連する疾患もしくは状態を処置すること、またはその疾患もしくは状態の可能性を低減させることを必要とする対象の神経細胞における、その疾患もしくは状態を処置するか、またはその疾患もしくは状態の可能性を低減させる方法が更に開示される。本方法は、STMN2タンパク質発現を増加させるアンチセンスオリゴヌクレオチドに神経細胞を接触させることを含み得る。
いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、潜在性エクソンをコードするSTMN2 RNA配列、プレRNA配列、または新生RNA配列に特異的に結合する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、5’スプライス部位、3’スプライス部位、または通常のTDP-43結合部位を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、一本鎖領域、例えば、TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、潜在性スプライス部位の近位部位、早期ポリアデニル化部位の近位部位、または潜在性スプライス部位と早期ポリアデニル化部位との間に位置する部位を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、構造化されていない潜在性エクソン内の標的領域に結合する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、TDP-43により調節される5’スプライス部位の近傍にまたはそれに隣接して結合する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、予測されるTDP-43結合部位の近位領域を標的とする。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、1つ以上のスプライス部位を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、正常長のまたはタンパク質をコードするSTMN2プレmRNAまたはmRNAを回復させる。
いくつかの実施形態では、対象は、ニューロンの成長及び修復の改善を示す。いくつかの実施形態では、疾患または状態は、神経変性疾患、例えば、筋萎縮性側索硬化症(ALS)、前頭側頭型認知症(FTD)、封入体筋炎(IBM)、パーキンソン病、またはアルツハイマー病である。いくつかの実施形態では、疾患または状態は、外傷性脳損傷である。いくつかの実施形態では、疾患または状態は、プロテアソーム阻害剤誘導性ニューロパチーである。いくつかの実施形態では、疾患または状態は、神経細胞におけるTDP-43のレベルの変異または低減に関連する。
いくつかの実施形態では、本方法は、有効量の第2の薬剤を対象に投与することを更に含む。いくつかの実施形態では、第2の薬剤は、神経変性疾患または外傷性脳損傷を処置するために投与される。いくつかの実施形態では、第2の薬剤は、STMN2(例えば、遺伝子治療薬として投与される)である。
本明細書では、TAR DNA結合タンパク質43(TDP-43)の機能性の減退に関連する疾患もしくは状態を処置すること、またはその疾患もしくは状態の可能性を低減させることを必要とする対象の神経細胞における、その疾患もしくは状態を処置するか、またはその疾患もしくは状態の可能性を低減させる方法もまた開示される。本方法は、STMN2タンパク質のレベルの低減を補正するアンチセンスオリゴヌクレオチドに神経細胞を接触させることを含み得、このアンチセンスオリゴヌクレオチドは、配列番号37~85からなる群から選択される配列を含む。
いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、配列番号37~74からなる群から選択される配列を含む。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含むか、またはより具体的には、アンチセンスオリゴヌクレオチドは、配列番号52を含み得る。特定の実施形態では、アンチセンスオリゴヌクレオチドは、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含むか、またはより具体的には、アンチセンスオリゴヌクレオチドは、配列番号73または配列番号53を含む。
本明細書では、TAR DNA結合タンパク質43(TDP-43)の機能性の減退に関連する疾患または状態の可能性を低減させることを必要とする対象の神経細胞における、その疾患または状態の可能性を低減させる方法が更に開示される。本方法は、STMN2 RNAへの潜在性エクソンの包含を抑制または防止する1つ以上のアンチセンスオリゴヌクレオチドに神経細胞を接触させることを含み得る。いくつかの実施形態では、1つ以上のアンチセンスオリゴヌクレオチドは、配列番号37~85からなる群から選択される配列を含む。
いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含むか、またはより具体的には、配列番号52を含む。特定の実施形態では、アンチセンスオリゴヌクレオチドは、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含むか、またはより具体的には、アンチセンスオリゴヌクレオチドは、配列番号73または配列番号53を含む。
いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、潜在性エクソンをコードするSTMN2 RNA配列、プレRNA配列、または新生RNA配列に特異的に結合する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、5’スプライス部位、3’スプライス部位、または通常のTDP-43結合部位を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、一本鎖領域、例えば、TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、潜在性スプライス部位の近位部位、早期ポリアデニル化部位の近位部位、または潜在性スプライス部位と早期ポリアデニル化部位との間に位置する部位を標的とするように設計されている。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、構造化されていない潜在性エクソン内の標的領域に結合する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、TDP-43により調節される5’スプライス部位の近傍にまたはそれに隣接して結合する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、予測されるTDP-43結合部位の近位領域を標的とする。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、TDP-43の通常の結合部位を標的とする。
いくつかの実施形態では、疾患または状態は、筋萎縮性側索硬化症(ALS)、前頭側頭型認知症(FTD)、封入体筋炎(IBM)、パーキンソン病、及びアルツハイマー病からなる群から選択される。いくつかの実施形態では、疾患または状態は、外傷性脳損傷である。いくつかの実施形態では、疾患または状態は、プロテアソーム阻害剤誘導性ニューロパチーである。
いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、潜在性スプライシングを抑制する。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、STMN2タンパク質の分解を防止するかまたは遅延させる。いくつかの実施形態では、対象は、ニューロンの成長及び修復の改善を示す。
いくつかの実施形態では、本方法は、有効量の第2の薬剤を対象に投与することを更に含む。いくつかの実施形態では、第2の薬剤は、神経変性疾患または外傷性脳損傷を処置するために投与される。
本明細書では、TAR DNA結合タンパク質43(TDP-43)の機能性の減退に関連する疾患もしくは状態を処置すること、またはその疾患もしくは状態の可能性を低減させることを必要とする対象の神経細胞における、その疾患もしくは状態を処置するか、またはその疾患もしくは状態の可能性を低減させる方法であって、STMN2タンパク質のレベルの低減を補正する多量体オリゴヌクレオチドに神経細胞を接触させることを含み、この多量体オリゴヌクレオチドが、配列番号37~85からなる群から選択される2つ以上のアンチセンスオリゴヌクレオチドを含む方法が、更に開示される。いくつかの実施形態では、多量体オリゴヌクレオチドは、配列番号37~74からなる群から選択される2つ以上のアンチセンスオリゴヌクレオチドを含む。
本明細書では、潜在性エクソン内の非構造化領域を標的とするように設計されている、STMN2タンパク質のレベルの低減を補正するアンチセンスオリゴヌクレオチドもまた開示される。いくつかの実施形態では、潜在性エクソン内の非構造化領域は、潜在性スプライス部位と早期ポリアデニル化部位との間に位置する。
本明細書では、対象におけるSTMN2またはELAVL3タンパク質のレベルの変化を検出する方法もまた開示される。本方法は、対象から試料を得ることと;STMN2またはELAVL3タンパク質レベルが変化しているか否かを検出することと、を含む。いくつかの実施形態では、対象は、筋萎縮性側索硬化症を有する。いくつかの実施形態では、STMN2またはELAVL3レベルが変化しているか否かを検出することは、STMN2またはELAVL3レベルが低下しているか否かを(例えば、ELISAを使用して)判定することを含む。いくつかの実施形態では、試料は、生体液試料(例えば、CSF試料)である。
本特許または出願書類は、カラーで作成された少なくとも1つの図面を含む。カラー図面を含む本特許または特許出願公開の複写は、要請及び必要な料金の支払により特許庁より提供されよう。
RNA結合タンパク質TDP-43の誤局在化または枯渇は、微小管調節因子をコードするSTMN2の発現低下をもたらす。STMN2は、正常な軸索の成長及び再生に不可欠である。TDP-43の機能低下により、STMN2タンパク質の発現低減をもたらす、不完全なまたは変化したSTMN2 RNA配列が生じる。STMN2は、有望な治療標的及び疾患リスク(例えば、神経変性疾患)のバイオマーカーである可能性がある。
本明細書に記載の研究は、STMN2 mRNAへの潜在性エクソンの包含を抑制または防止するための組成物及び方法に関する。STMN2 mRNAへの潜在性エクソンの包含により、トランケートされた転写物及びタンパク質がもたらされる可能性がある。いくつかの態様では、潜在性エクソンの包含は、早期ポリアデニル化をもたらす。STMN2の発現は、TDP-43が隔離されたときまたはその機能が低減したときに生じるSTMN2の潜在性スプライシング形態の抑制を通じて、(例えば、アンチセンスオリゴヌクレオチドの投与により)潜在性形態の出現または蓄積を遮断して、それを機能的なSTMN2 RNAへと再度変換するか、またはそれを回復させることなどによって、回復させることができる。更に、本明細書に記載の研究は、STMN2のタンパク質合成を増加させる、すなわちSTMN2タンパク質発現を増加させるための組成物及び方法に関する。
薬剤及び医薬組成物
本開示は、TDP-43の機能が減退しているかまたはTDP病変が存在する場合に発生しかつ存在量が増加するSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、それにより不完全なまたは変化したSTMN2 RNA配列の包含を抑制または防止する薬剤(例えば、アンチセンスオリゴヌクレオチド)を企図する。いくつかの態様では、薬剤は、STMN2タンパク質の分解を防止する。いくつかの態様では、薬剤は、STMN2タンパク質レベルを回復させる。いくつかの態様では、薬剤は、STMN2 RNAへの潜在性エクソンの包含を抑制または防止する。特定の態様では、薬剤は、潜在性エクソンをコードするSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合する。
本開示は、TDP-43の機能が減退しているかまたはTDP病変が存在する場合に発生しかつ存在量が増加するSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、それにより不完全なまたは変化したSTMN2 RNA配列の包含を抑制または防止する薬剤(例えば、アンチセンスオリゴヌクレオチド)を企図する。いくつかの態様では、薬剤は、STMN2タンパク質の分解を防止する。いくつかの態様では、薬剤は、STMN2タンパク質レベルを回復させる。いくつかの態様では、薬剤は、STMN2 RNAへの潜在性エクソンの包含を抑制または防止する。特定の態様では、薬剤は、潜在性エクソンをコードするSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合する。
いくつかの態様では、本開示は、ELAVL3 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合する薬剤(例えば、アンチセンスオリゴヌクレオチド)を更に企図する。ELAVL3は、TDP-43の機能が減退しているかまたはTDP病変が存在する場合にダウンレギュレートされ得る。いくつかの態様では、薬剤は、ELAVL3の潜在性スプライシングを抑制または防止する。
いくつかの実施形態では、薬剤(例えば、アンチセンスオリゴヌクレオチド)は、STMN2 RNA配列(例えば、不完全なまたは変化したSTMN2 RNA配列)に結合する。いくつかの態様では、短く不完全なまたは変化したSTMN2 RNA配列へ薬剤が結合すると、RNAポリメラーゼによって継続的に生成されるようになる。例えば、薬剤は、潜在性エクソンのポリアデニル化部位での早期転写終結を直接抑制し得るか、またはその標的部位でのTDP-43結合の活性を模倣することにより、潜在性エクソンでの転写終結を変化させ得る。いくつかの態様では、薬剤は、STMN2 RNAへの潜在性エクソンの包含を抑制または防止する。いくつかの態様では、薬剤は、STMN2タンパク質の分解を防止する。いくつかの態様では、薬剤は、(例えば、エクソンスキッピングを通じて)STMN2レベルを増加させる。いくつかの態様では、薬剤は、正常長のまたはタンパク質をコードするSTMN2 RNA(例えば、プレmRNAまたはmRNA)を回復させる。いくつかの態様では、薬剤は、STMN2 RNAの量または活性を増加させる。いくつかの態様では、薬剤は、STMN2のタンパク質発現を増加させる。
「増加した」または「増加する」という用語は、本明細書では概して、統計学的に有意な量の増加を意味するために使用される。疑義を避けるために述べると、「増加した」または「増加する」という用語は、参照レベルと比較して少なくとも10%の増加、例えば、参照レベルと比較して少なくとも約20%、もしくは少なくとも約30%、もしくは少なくとも約40%、もしくは少なくとも約50%、もしくは少なくとも約60%、もしくは少なくとも約70%、もしくは少なくとも約80%、もしくは少なくとも約90%の増加、もしくは100%までの増加、または10~100%の間の任意の増加、あるいは参照レベルと比較して少なくとも約2倍、もしくは少なくとも約3倍、もしくは少なくとも約4倍、もしくは少なくとも約5倍、もしくは少なくとも約10倍の増加、または2倍~10倍以上の間の任意の増加を意味する。
いくつかの態様では、薬剤は、STMN2 RNAの量または活性を、少なくとも約2倍、少なくとも約3倍、少なくとも約4倍、少なくとも約5倍、少なくとも約6倍、少なくとも約7倍、少なくとも約8倍、少なくとも約9倍、または少なくとも約10倍増加させる。いくつかの態様では、薬剤は、STMN2タンパク質発現を、少なくとも約2倍、少なくとも約3倍、少なくとも約4倍、少なくとも約5倍、少なくとも約6倍、少なくとも約7倍、少なくとも約8倍、少なくとも約9倍、または少なくとも約10倍増加させる。
いくつかの実施形態では、薬剤(例えば、アンチセンスオリゴヌクレオチド)は、1つ以上の部位、例えば、STMN2転写物の5’スプライス部位、3’スプライス部位、通常の結合部位、及び/またはポリアデニル化部位を標的とする。いくつかの態様では、薬剤は、1つ以上の部位、例えば、STMN2転写物の5’スプライス部位の近位部位、3’スプライス部位の近位部位、通常の結合部位の近位部位、及び/またはポリアデニル化部位の近位部位を標的とする。特定の実施形態では、薬剤は、TDP-43により調節される5’スプライス部位、TDP-43の通常の結合部位、及び/または潜在性ポリアデニル化部位を含む、1つ以上の部位を標的とする。いくつかの実施形態では、薬剤は、一本鎖部位を標的とする。特定の実施形態では、薬剤は、TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とする。いくつかの実施形態では、薬剤は、潜在性スプライス部位の近位部位を標的とする。いくつかの実施形態では、薬剤は、早期ポリアデニル化部位の近位部位を標的とする。いくつかの実施形態では、薬剤は、潜在性スプライス部位と早期ポリアデニル化部位との間に位置する領域を標的とする。いくつかの実施形態では、薬剤は、ポリアデニル化部位を標的としないか、またはそれに結合しない。いくつかの実施形態では、薬剤は、STMN2転写物のポリアデニル化部位を標的としないか、またはそれに結合しない。いくつかの実施形態では、薬剤は、潜在性ポリアデニル化部位を標的としないか、またはそれに結合しない。いくつかの態様では、薬剤は、STMN2エクソン2からエクソン1へのスプライシングを標的とし、促進する。
STMN2エクソン1は、
AGCTCCTAGGAAGCTTCAGGGCTTAAAGCTCCACTCTACTTGGACTGTACTATCAGGCCCCCAAAATGGGGGGAGCCGACAGGGAAGGACTGATTTCCATTTCAAACTGCATTCTGGTACTTTGTACTCCAGCACCATTGGCCGATCAATATTTAATGCTTGGAGATTCTGACTCTGCGGGAGTCATGTCAGGGGACCTTGGGAGCCAATCTGCTTGAGCTTCTGAGTGATAATTATTCATGGGCTCCTGCCTCTTGCTCTTTCTCTAGCACGGTCCCACTCTGCAGACTCAGTGCCTTATTCAGTCTTCTCTCTCGCTCTCTCCGCTGCTGTAGCCGGACCCTTTGCCTTCGCCACTGCTCAGCGTCTGCACATCCCTACAATGGCTAAAACAGCAATGGGACTCGGCAGAAGACCTTCGAGAGAAAGGTAGAAAATAAGAATTTGGCTCTCTGTGTGAGCATGTGTGCGTGTGTGCGAGAGAGAGAGACAGACAGCCTGCCTAAGAAGAAATGAATGTGAATGCGGCTTGTGGCACAGTTGACAAGGATGATAAATCAATAATGCAAGCTTACTATCATTTATGAATAGC(配列番号1)の配列を有し得る。
AGCTCCTAGGAAGCTTCAGGGCTTAAAGCTCCACTCTACTTGGACTGTACTATCAGGCCCCCAAAATGGGGGGAGCCGACAGGGAAGGACTGATTTCCATTTCAAACTGCATTCTGGTACTTTGTACTCCAGCACCATTGGCCGATCAATATTTAATGCTTGGAGATTCTGACTCTGCGGGAGTCATGTCAGGGGACCTTGGGAGCCAATCTGCTTGAGCTTCTGAGTGATAATTATTCATGGGCTCCTGCCTCTTGCTCTTTCTCTAGCACGGTCCCACTCTGCAGACTCAGTGCCTTATTCAGTCTTCTCTCTCGCTCTCTCCGCTGCTGTAGCCGGACCCTTTGCCTTCGCCACTGCTCAGCGTCTGCACATCCCTACAATGGCTAAAACAGCAATGGGACTCGGCAGAAGACCTTCGAGAGAAAGGTAGAAAATAAGAATTTGGCTCTCTGTGTGAGCATGTGTGCGTGTGTGCGAGAGAGAGAGACAGACAGCCTGCCTAAGAAGAAATGAATGTGAATGCGGCTTGTGGCACAGTTGACAAGGATGATAAATCAATAATGCAAGCTTACTATCATTTATGAATAGC(配列番号1)の配列を有し得る。
STMN2エクソン2は、
CCTACAAGGAAAAAATGAAGGAGCTGTCCATGCTGTCACTGATCTGCTCTTGCTTTTACCCGGAACCTCGCAACATCAACATCTATACTTACGATGG(配列番号2)の配列を有し得る。
CCTACAAGGAAAAAATGAAGGAGCTGTCCATGCTGTCACTGATCTGCTCTTGCTTTTACCCGGAACCTCGCAACATCAACATCTATACTTACGATGG(配列番号2)の配列を有し得る。
潜在性エクソンは、GACTCGGCAGAAGACCTTCGAGAGAAAGGTAGAAAATAAGAATTTGGCTCTCTGTGTGAGCATGTGTGCGTGTGTGCGAGAGAGAGAGACAGACAGCCTGCCTAAGAAGAAATGAATGTGAATGCGGCTTGTGGCACAGTTGACAAGGATGATAAATCAATAATGCAAGCTTACTATCATTTATGAATAGC(配列番号3)の配列を有し得る。
使用することができる薬剤の例示的なタイプとしては、有機小分子または無機小分子;サッカリン;オリゴ糖;多糖;ペプチド、タンパク質、ペプチド類似体及び誘導体からなる群から選択される生体高分子;ペプチド模倣物;siRNA、shRNA、アンチセンスRNA、リボザイム、及びアプタマーからなる群から選択される核酸;細菌、植物、真菌、動物細胞、及び動物組織からなる群から選択される生体物質から作製される抽出物;天然に存在する組成物または合成組成物;抗体;ならびにこれらの任意の組み合わせが挙げられる。
いくつかの実施形態では、薬剤は、オリゴヌクレオチド、タンパク質、または小分子である。いくつかの実施形態では、薬剤は、1つ以上のオリゴヌクレオチドを含む。いくつかの態様では、オリゴヌクレオチドは、スプライススイッチングオリゴヌクレオチドである。特定の態様では、オリゴヌクレオチドは、アンチセンスオリゴヌクレオチド(ASO)である。いくつかの実施形態では、薬剤は、アンチセンスオリゴヌクレオチドではない。いくつかの実施形態では、薬剤は、標的部位(例えば、STMN2転写物)に結合して標的の代謝をシフトさせることができる小分子(例えば、ブラナプラム(Novartis)またはリスジプラム(Roche))である。
いくつかの実施形態では、薬剤は、オリゴヌクレオチド、タンパク質、または小分子である。いくつかの実施形態では、薬剤は、1つ以上のオリゴヌクレオチドを含む。複数のオリゴヌクレオチドを含む薬剤は、多量体化合物と見なされ得る。いくつかの態様では、薬剤は、オリゴヌクレオチドの1つ以上のコピーを含む。いくつかの態様では、薬剤は、複数のオリゴヌクレオチドの1つ以上のコピーを含む。いくつかの態様では、複数のオリゴヌクレオチドは共有結合され得る。いくつかの態様では、オリゴヌクレオチドは、スプライススイッチングオリゴヌクレオチドである。特定の態様では、オリゴヌクレオチドは、アンチセンスオリゴヌクレオチド(ASO)である。いくつかの実施形態では、薬剤は、標的部位(例えば、STMN2転写物)に結合して標的の代謝をシフトさせることができる小分子(例えば、ブラナプラム(Novartis)またはリスジプラム(Roche))である。いくつかの態様では、薬剤は、毒性、例えば血小板毒性を呈さない。
薬剤は、5’スプライス部位、3’スプライス部位、通常の結合部位、またはポリアデニル化部位のうちの1つ以上を標的とし得る。いくつかの態様では、薬剤は、STMN2転写物の5’スプライス部位の近位部位、3’スプライス部位の近位部位、通常の結合部位の近位部位、及び/またはポリアデニル化部位の近位部位のうちの1つ以上を標的とする。いくつかの実施形態では、薬剤は、潜在性スプライス部位の近位部位を標的とする。いくつかの実施形態では、薬剤は、早期ポリアデニル化部位の近位部位を標的とする。いくつかの実施形態では、薬剤は、STMN2転写物の一本鎖領域を標的とする。いくつかの実施形態では、薬剤は、TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とする。いくつかの実施形態では、薬剤は、潜在性スプライス部位と早期ポリアデニル化部位との間に位置する領域を標的とする。いくつかの態様では、ポリアデニル化部位は、STMN2転写物のポリアデニル化部位である。いくつかの態様では、ポリアデニル化部位は、潜在性エクソンのポリアデニル化部位である(例えば、潜在性ポリアデニル化部位である)。いくつかの実施形態では、薬剤は、5’スプライス部位(例えば、TDP-43の5’スプライス部位)を標的としない。いくつかの実施形態では、薬剤は、通常の結合部位(例えば、通常のTDP-43結合部位)を標的としない。いくつかの実施形態では、薬剤は、ポリアデニル化部位(例えば、潜在性ポリアデニル化部位)を標的としない。いくつかの態様では、
特定の実施形態では、アンチセンスオリゴヌクレオチドは、5’スプライス部位、3’スプライス部位、通常の結合部位、またはポリアデニル化部位のうちの1つ以上を標的とし得る。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、5’スプライス部位(例えば、TDP-43の5’スプライス部位)を標的としない。特定の態様では、アンチセンスオリゴヌクレオチドは、STMN2転写物の5’スプライス部位の近位部位、3’スプライス部位の近位部位、通常の結合部位の近位部位、及び/またはポリアデニル化部位の近位部位のうちの1つ以上を標的とする。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、STMN2転写物の一本鎖領域を標的とする。特定の実施形態では、アンチセンスオリゴヌクレオチドは、TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とする。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、潜在性スプライス部位の近位部位を標的とする(例えば、潜在性スプライス部位から-1の部位を標的とする)。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、早期ポリアデニル化部位の近位部位を標的とする。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、潜在性スプライス部位と早期ポリアデニル化部位との間に位置する領域を標的とする。いくつかの態様では、アンチセンスオリゴヌクレオチドは、潜在性スプライスジャンクションを基準として+90~+105、またはより具体的には+94または+101の領域を標的とする。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、通常の結合部位(例えば、通常のTDP-43結合部位)を標的としない。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、ポリアデニル化部位(例えば、潜在性ポリアデニル化部位)を標的としない。
特定の実施形態では、アンチセンスオリゴヌクレオチドは、配列番号37~85からなる群から選択される配列を含む。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、配列番号37~74からなる群から選択される配列を含む。いくつかの態様では、アンチセンスオリゴヌクレオチドは、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含む。特定の態様では、アンチセンスオリゴヌクレオチドは、配列番号52を含む。いくつかの実施形態では、アンチセンスオリゴヌクレオチドは、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含む。一実施形態では、アンチセンスオリゴヌクレオチドは、配列番号73を含む。一実施形態では、アンチセンスオリゴヌクレオチドは、配列番号53を含む。一実施形態では、アンチセンスオリゴヌクレオチドは、配列番号72を含む。
表1は、例示的なアンチセンスオリゴヌクレオチドのリストを示し、場合によっては、STMN2イントロン内の対応する標的部位を示す。配列番号93~108内の下線付きの塩基は、潜在性スプライス部位に隣接する塩基を表す。配列番号112~114内の下線付きの塩基は、TDP-43タンパク質の結合部位を表す。本明細書に記載のオリゴヌクレオチドは、複数の化学修飾により合成された。例えば、配列番号37~74のアンチセンスオリゴヌクレオチドは、以下の構造:
を有するMOE糖及びホスホロチオエート結合により完全に修飾された。追加の修飾を試験することもできる。
を有するMOE糖及びホスホロチオエート結合により完全に修飾された。追加の修飾を試験することもできる。
オリゴヌクレオチド(例えば、アンチセンスオリゴヌクレオチド)を、5’キャップでのリボソーム会合を防止するか、mRNA成熟化の間のポリアデニル化を防止するか、またはスプライシング事象に影響を及ぼすmRNA領域に結合するように設計することができる(それぞれ参照により本明細書に組み込まれる、Bennett and Swayze,Annu.Rev.Phamacol.Toxicol.,2010、Watts and Corey,J.Pathol.,2012、Kole et al.,Nat.Rev.Drug Discov.,2012、Saleh et al,In Exon Skipping:Methods and Protocols,2012)。いくつかの態様では、オリゴヌクレオチド(例えば、アンチセンスオリゴヌクレオチド)は、例えば、5’TDP-3スプライス部位、またはTDP-43の通常の結合部位を含む、1つ以上の部位を標的とするように設計されている。いくつかの態様では、オリゴヌクレオチドは、1つ以上のスプライス部位を標的とする。いくつかの態様では、オリゴヌクレオチドは、TDP-43により調節される5’スプライス部位またはTDP-43の通常の結合部位のうちの1つ以上を標的とする。いくつかの態様では、アンチセンスオリゴヌクレオチドは、ポリアデニル化部位(例えば、潜在性ポリアデニル化部位)を標的としないように設計されている。いくつかの態様では、オリゴヌクレオチドは、潜在性スプライス部位とポリアデニル化部位との間に位置する非構造化領域を標的とする(図83を参照されたい)。
アンチセンスオリゴヌクレオチドは、ワトソン-クリック塩基対形成によってRNA転写物を標的とし、タンパク質発現の低減または修飾をもたらすことができる、DNAの小さな配列(例えば、約8~50塩基対長)である。オリゴヌクレオチドは、リン酸骨格及び糖環で構成されている。いくつかの実施形態では、オリゴヌクレオチドは修飾されていない。他の実施形態では、オリゴヌクレオチドは、例えば、アンチセンスオリゴヌクレオチドの溶解性、結合性、効力、及び/または安定性を向上させるための、1つ以上の修飾を含む。修飾オリゴヌクレオチドは、非修飾RNAまたはDNAに対して少なくとも1つの修飾を含み得る。いくつかの実施形態では、オリゴヌクレオチドは、ヌクレオシド間結合修飾、糖修飾、及び/または核酸塩基修飾を含むように修飾される。そのような修飾の例は、当業者に公知である。
いくつかの実施形態では、オリゴヌクレオチドは、少なくとも1つのヌクレオチドを修飾ヌクレオチドで置換することによって修飾され、その結果、in vivo安定性が、対応する非修飾オリゴヌクレオチドと比較して増強される。いくつかの態様では、修飾ヌクレオチドは、糖修飾ヌクレオチドである。別の態様では、修飾ヌクレオチドは、核酸塩基修飾ヌクレオチドである。
いくつかの実施形態では、オリゴヌクレオチドは、少なくとも1つの修飾ヌクレオチド類似体を含有し得る。ヌクレオチド類似体は、例えば、オリゴヌクレオチド分子の5’末端及び/または3’末端の領域中の、標的特異的活性、例えば、スプライス部位選択調節活性が実質的に影響されない位置に位置し得る。いくつかの態様では、末端は、修飾ヌクレオチド類似体を導入することによって安定化され得る。
いくつかの態様では、好ましいヌクレオチド類似体には、糖修飾及び/または骨格修飾リボヌクレオチドが含まれる(すなわち、リン酸-糖骨格への修飾が含まれる)。例えば、リボヌクレオチドのホスホジエステル結合は、窒素または硫黄ヘテロ原子のうちの少なくとも1つを含むように修飾され得る。好ましい骨格修飾リボヌクレオチドにおいて、隣接するリボヌクレオチドに連結するリン酸エステル基は、修飾基、例えば、ホスホチオエート基の修飾基によって置換される。好ましい糖修飾リボヌクレオチドにおいて、2’-OH基は、H、OR、R、ハロ、SH、SR、NH2、NHR、NR2またはONから選択される基(式中、RはC1~C6アルキル、アルケニルまたはアルキニルであり、ハロはF、Cl、BrまたはIである)によって置換される。
いくつかの実施形態では、修飾オリゴヌクレオチドは、修飾糖部分を含む1つ以上の修飾ヌクレオシドを含む。いくつかの実施形態では、修飾オリゴヌクレオチドは、修飾核酸塩基を含む1つ以上の修飾ヌクレオシドを含む。いくつかの実施形態では、修飾オリゴヌクレオチドは、1つ以上の修飾ヌクレオシド間結合を含む。特定の実施形態では、修飾オリゴヌクレオチドは、修飾糖部分を含む1つ以上の修飾ヌクレオシド、修飾核酸塩基を含む1つ以上の修飾ヌクレオシド、及び1つ以上の修飾ヌクレオシド間結合のうちの少なくとも2つを含む。特定の実施形態では、修飾オリゴヌクレオチドは、修飾糖部分を含む1つ以上の修飾ヌクレオシド、修飾核酸塩基を含む1つ以上の修飾ヌクレオシド、及び1つ以上の修飾ヌクレオシド間結合を含む。
糖修飾
いくつかの実施形態では、修飾糖部分は、非二環式修飾糖部分である。いくつかの実施形態では、修飾糖部分は、二環式または三環式糖部分である。いくつかの実施形態では、修飾糖部分は、糖代替物である。そのような糖代替物は、他のタイプの修飾糖部分の置換に対応する1つ以上の置換を含み得る。
いくつかの実施形態では、修飾糖部分は、非二環式修飾糖部分である。いくつかの実施形態では、修飾糖部分は、二環式または三環式糖部分である。いくつかの実施形態では、修飾糖部分は、糖代替物である。そのような糖代替物は、他のタイプの修飾糖部分の置換に対応する1つ以上の置換を含み得る。
いくつかの実施形態では、修飾糖部分は、1つ以上の置換基を有するフラノシル環であって、その置換基のいずれもフラノシル環の2つの原子を架橋して二環式構造を形成しないフラノシル環を含む、非二環式修飾糖部分である。そのような非架橋置換基は、2’位、4’位及び/または5’位の置換基を含むがこれらに限定されない、フラノシルの任意の位置に存在し得る。特定の実施形態では、非二環式修飾糖部分の1つ以上の非架橋置換基は、分枝状である。
いくつかの実施形態では、修飾糖部分は、フラノシル環の2つの原子を架橋して第2の環を形成し二環式糖部分を生じさせる置換基を含む。いくつかの態様では、二環式糖部分は、4’フラノース環原子と2’フラノース環原子との間に架橋を含む。
いくつかの態様では、二環式糖部分及びそのような二環式糖部分を組み込むヌクレオシドは、異性体配置により更に定義される。いくつかの実施形態では、LNAヌクレオシドは、α-L配置で存在する。いくつかの実施形態では、LNAヌクレオシドは、β-D配置で存在する。
いくつかの実施形態では、オリゴヌクレオチド修飾は、2’-ヒドロキシル基が糖環の3’または4’炭素原子に連結され、それにより二環式糖部分を形成するロックド核酸(LNA)を含む。結合は、好ましくは2’酸素原子と4’炭素原子とを架橋するメチレン(-CH2-)n基である(式中、nは1または2である)。LNA及びその調製はWO98/39352及びWO99/14226に記載されており、その全内容は、参照により本明細書に組み込まれる。
いくつかの実施形態では、修飾糖部分は、1つ以上の非架橋糖置換基及び1つ以上の架橋糖置換基(例えば、5’で置換され4’-2’で架橋された糖)を含む。
いくつかの実施形態では、修飾糖部分は、糖代替物である。いくつかの態様では、糖部分の酸素原子は、例えば、硫黄、炭素または窒素原子によって置換されている。いくつかの態様では、そのような修飾糖部分はまた、本明細書に記載の架橋及び/または非架橋置換基も含む。いくつかの態様では、糖代替物は、5つ以外の原子を有する環を含む。特定の態様では、糖代替物は、6員のテトラヒドロピラン(「THP」)を含む。いくつかの態様では、糖代替物は、非環式部分を含む。
核酸塩基修飾
修飾オリゴヌクレオチドは、非修飾核酸塩基を含む1つ以上のヌクレオシドを含み得る。いくつかの実施形態では、修飾オリゴヌクレオチドは、修飾核酸塩基を含む1つ以上のヌクレオシドを含む。いくつかの実施形態では、修飾オリゴヌクレオチドは、核酸塩基を含まない1つ以上のヌクレオシドを含む。
修飾オリゴヌクレオチドは、非修飾核酸塩基を含む1つ以上のヌクレオシドを含み得る。いくつかの実施形態では、修飾オリゴヌクレオチドは、修飾核酸塩基を含む1つ以上のヌクレオシドを含む。いくつかの実施形態では、修飾オリゴヌクレオチドは、核酸塩基を含まない1つ以上のヌクレオシドを含む。
特定の実施形態では、修飾核酸塩基は、5-置換ピリミジン、6-アザピリミジン、アルキルまたはアルキニル置換ピリミジン、アルキル置換プリン、ならびにN-2、N-6、及びO-6置換プリンから選択される。特定の実施形態では、修飾核酸塩基は、2-アミノプロピルアデニン、5-ヒドロキシメチルシトシン、キサンチン、ヒポキサンチン、2-アミノアデニン、6-N-メチルグアニン、6-N-メチルアデニン、2-プロピルアデニン、2-チオウラシル、2-チオチミン及び2-チオシトシン、5-プロピニル(-C℃-C]3/4)ウラシル、5-プロピニルシトシン、6-アゾウラシル、6-アゾシトシン、6-アゾチミン、5-リボシルウラシル(シュードウラシル)、4-チオウラシル、8-ハロ、8-アミノ、8-チオール、8-チオアルキル、8-ヒドロキシル、8-アザ及び他の8-置換プリン、5-ハロ(特に、5-ブロモ、5-トリフルオロメチル、5-ハロウラシル、及び5-ハロシトシン)、7-メチルグアニン、7-メチルアデニン、2-F-アデニン、2-アミノアデニン、7-デアザグアニン、7-デアザアデニン、3-デアザグアニン、3-デアザアデニン、6-N-ベンゾイルアデニン、2-N-イソブチリルグアニン、4-N-ベンゾイルシトシン、4-N-ベンゾイルウラシル、5-メチル4-N-ベンゾイルシトシン、5-メチル4-N-ベンゾイルウラシル、ユニバーサル塩基、疎水性塩基、無差別塩基(promiscuous base)、サイズ拡張塩基(size-expanded base)ならびにフッ素化塩基から選択される。更なる修飾核酸塩基としては、三環式ピリミジン、例えば、1,3-ジアザフェノキサジン-2-オン、1,3-ジアザフェノチアジン-2-オン、及び9-(2-アミノエトキシ)-1,3-ジアザフェノキサジン-2-オン(G-クランプ)が挙げられる。修飾核酸塩基には、プリン塩基またはピリミジン塩基が他の複素環で置換されているもの、例えば7-デアザ-アデニン、7-デアザグアノシン、2-アミノピリジン、及び2-ピリドンも含まれ得る。
また、核酸塩基修飾リボヌクレオチド、すなわち、天然に存在する核酸塩基の代わりに少なくとも1つの天然に存在しない核酸塩基を含有するリボヌクレオチドも好ましい。修飾核酸塩基の例としては、5位でのウリジン及び/またはシチジン修飾、例えば、5-(2-アミノ)プロピルウリジン、5-ブロモウリジン;8位で修飾されたアデノシン及び/またはグアノシン、例えば、8-ブロモグアノシン;デアザヌクレオチド、例えば、7-デアザ-アデノシン;O-アルキル化及びN-アルキル化ヌクレオチド、例えば、N6-メチルアデノシンが挙げられるが、これらに限定されない。本発明のオリゴヌクレオチド試薬はまた、オリゴヌクレオチド試薬のin vivo薬理学的特性を向上させる化学的部分で修飾され得る。
ヌクレオシド間修飾
いくつかの実施形態では、修飾オリゴヌクレオチドのヌクレオシドは、任意のヌクレオシド間結合を使用して一緒に連結される。ヌクレオシド間結合基の2つの主なクラスは、リン原子の有無により定義される。代表的なリン含有ヌクレオシド間結合としては、ホスホジエステル結合(「P=O」)(非修飾結合または天然に存在する結合とも称される)を含むリン酸、ホスホトリエステル、メチルホスホネート、ホスホロアミダート、及びホスホロチオエート(「P=S」)、及びホスホロジチオエート(「HS-P=S」)が挙げられるが、これらに限定されない。代表的な非リン含有ヌクレオシド間結合基としては、メチレンメチルイミノ(-CH2-N(CH3)-O-CH2-)、チオジエステル、チオノカルバメート(-O-C(=O)(NH)-S-);シロキサン(-O-SiH2-O-);及びN,N’-ジメチルヒドラジン(-CH2-N(CH3)-N(CH3)-)が挙げられるが、これらに限定されない。修飾ヌクレオシド間結合は、天然に存在するリン酸結合と比較して、オリゴヌクレオチドのヌクレアーゼ耐性を変化させる(通常は増加させる)ために使用することができる。特定の実施形態では、キラル原子を有するヌクレオシド間結合を、ラセミ混合物として、または別個の鏡像異性体として調製することができる。リン含有及び非リン含有ヌクレオシド間結合を調製する方法は、当業者に周知である。
いくつかの実施形態では、修飾オリゴヌクレオチドのヌクレオシドは、任意のヌクレオシド間結合を使用して一緒に連結される。ヌクレオシド間結合基の2つの主なクラスは、リン原子の有無により定義される。代表的なリン含有ヌクレオシド間結合としては、ホスホジエステル結合(「P=O」)(非修飾結合または天然に存在する結合とも称される)を含むリン酸、ホスホトリエステル、メチルホスホネート、ホスホロアミダート、及びホスホロチオエート(「P=S」)、及びホスホロジチオエート(「HS-P=S」)が挙げられるが、これらに限定されない。代表的な非リン含有ヌクレオシド間結合基としては、メチレンメチルイミノ(-CH2-N(CH3)-O-CH2-)、チオジエステル、チオノカルバメート(-O-C(=O)(NH)-S-);シロキサン(-O-SiH2-O-);及びN,N’-ジメチルヒドラジン(-CH2-N(CH3)-N(CH3)-)が挙げられるが、これらに限定されない。修飾ヌクレオシド間結合は、天然に存在するリン酸結合と比較して、オリゴヌクレオチドのヌクレアーゼ耐性を変化させる(通常は増加させる)ために使用することができる。特定の実施形態では、キラル原子を有するヌクレオシド間結合を、ラセミ混合物として、または別個の鏡像異性体として調製することができる。リン含有及び非リン含有ヌクレオシド間結合を調製する方法は、当業者に周知である。
更なる修飾は当業者に公知であり、例をWO2019/241648、US10,307,434、US9,045,518、及びUS10,266,822に見ることができ、これらの各々は参照により本明細書に組み込まれる。
オリゴヌクレオチドは、不完全なまたは変化したSTMN2 RNAを標的とするのに十分な任意のサイズ及び/または化学組成であり得る。いくつかの実施形態では、オリゴヌクレオチドは、約5~300ヌクレオチドまたは修飾ヌクレオチドである。いくつかの態様では、オリゴヌクレオチドは、約10~100、15~85、20~70、25~55、または30~40ヌクレオチドまたは修飾ヌクレオチドである。特定の態様では、オリゴヌクレオチドは、約15~35、15~20、20~25、25~30、または30~35ヌクレオチドまたは修飾ヌクレオチドである。
いくつかの実施形態では、オリゴヌクレオチド及び標的RNA配列(例えば、不完全なまたは変化したSTMN2 RNA)は100%の配列相補性を有する。いくつかの態様では、オリゴヌクレオチドは、標的配列と比較して、配列変動、例えば、挿入、欠失、及び単一点変異を含み得る。いくつかの実施形態では、オリゴヌクレオチドは、標的RNA(例えば、STMN2 mRNA、プレmRNA、または新生RNA)に対して少なくとも70%の配列同一性または相補性を有する。特定の実施形態では、オリゴヌクレオチドは、標的配列に対して少なくとも70%、75%、80%、85%、90%、95%、97%、99%、または100%の配列同一性を有する。
不完全なまたは変化したSTMN2 RNA配列(例えば、STMN2 mRNA配列、プレmRNA配列、または新生RNA配列)を標的とするアンチセンスオリゴヌクレオチドは、当業者に公知の任意の方法によって設計され得る。特定の態様では、1つ以上のオリゴヌクレオチドが合成される。
いくつかの実施形態では、STMN2は、遺伝子治療薬として投与される。いくつかの実施形態では、STMN2は、本明細書に記載の薬剤と併用投与される。
いくつかの実施形態では、薬剤は、c-Jun N末端キナーゼ(JNK)の阻害剤である。いくつかの態様では、JNK阻害剤は、有機小分子または無機小分子;サッカリン;オリゴ糖;多糖;ペプチド、タンパク質、ペプチド類似体及び誘導体からなる群から選択される生体高分子;ペプチド模倣物;siRNA、shRNA、アンチセンスRNA、リボザイム、及びアプタマーからなる群から選択される核酸;細菌、植物、真菌、動物細胞、及び動物組織からなる群から選択される生体物質から作製される抽出物;天然に存在する組成物または合成組成物;抗体;ならびにこれらの任意の組み合わせからなる群から選択される。特定の態様では、薬剤は、小分子阻害剤、オリゴヌクレオチド(例えば、JNKの発現を低減させるように設計されたもの)、または遺伝子治療薬(例えば、JNKを阻害するように設計されたもの)である。いくつかの態様では、JNKの阻害は、STMN2タンパク質レベルを回復または増加させる。特定の実施形態では、薬剤は、JNKを標的とするオリゴヌクレオチド(例えば、アンチセンスオリゴヌクレオチド)である。
本開示は更に、不完全なまたは変化したSTMN2 RNA配列に結合する薬剤(例えば、アンチセンスオリゴヌクレオチド)を含む医薬組成物を企図する。いくつかの実施形態では、医薬組成物は、潜在性エクソンをコードするSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に結合する薬剤を含む。いくつかの実施形態では、医薬組成物は、STMN2タンパク質の分解を防止する薬剤を含む。いくつかの実施形態では、医薬組成物は、STMN2タンパク質の発現を増加させる、例えば、STMN2タンパク質の発現を活性化する薬剤を含む。いくつかの態様では、組成物は、オリゴヌクレオチド、タンパク質、または小分子を含む。いくつかの実施形態では、組成物は、潜在性エクソンをコードするSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合するオリゴヌクレオチド(例えば、アンチセンスオリゴヌクレオチド)を含む。いくつかの態様では、薬剤(例えば、アンチセンスオリゴヌクレオチド)は、STMN2 RNAへの潜在性エクソンの包含を抑制または防止する。いくつかの態様では、薬剤は、潜在性スプライシングを抑制する。
いくつかの実施形態では、医薬組成物は、1つ以上の部位、例えば、1つ以上のスプライス部位、結合部位、またはポリアデニル化部位を標的とする薬剤(例えば、アンチセンスオリゴヌクレオチド)を含む。いくつかの実施形態では、医薬組成物は、1つ以上のスプライス部位(例えば、TDP-43により調節される5’スプライス部位)を標的とする薬剤を含む。いくつかの実施形態では、医薬組成物は、通常の結合部位(例えば、通常のTDP-43結合部位)を標的とする薬剤を含む。いくつかの実施形態では、医薬組成物は、ポリアデニル化部位(例えば、潜在性ポリアデニル化部位)を標的とする薬剤を含む。いくつかの実施形態では、医薬組成物は、潜在性スプライス部位の近位部位またはポリアデニル化部位(例えば、早期ポリアデニル化部位)の近位部位を標的とする薬剤を含む。いくつかの実施形態では、医薬組成物は、潜在性スプライス部位とポリアデニル化部位との間に位置する部位を標的とする薬剤を含む。いくつかの実施形態では、医薬組成物は、1つ以上のスプライス部位(例えば、TDP-43により調節される5’スプライス部位)を標的としない薬剤を含む。いくつかの実施形態では、医薬組成物は、通常の結合部位(例えば、通常のTDP-43結合部位)を標的としない薬剤を含む。いくつかの実施形態では、医薬組成物は、ポリアデニル化部位(例えば、潜在性ポリアデニル化部位)を標的としない薬剤を含む。
いくつかの態様では、医薬組成物は、多量体化合物、例えば、2つ以上のアンチセンスオリゴヌクレオチドを含む化合物を含む。2つ以上のアンチセンスオリゴヌクレオチドは、同じ配列を有する2つ以上のアンチセンスオリゴヌクレオチドを含んでもよく、または代わりに、異なる配列を有する2つ以上のアンチセンスオリゴヌクレオチドを含んでもよい。いくつかの態様では、2つ以上のアンチセンスオリゴヌクレオチドは、共有結合されている。いくつかの態様では、医薬組成物は、2つ以上のアンチセンスオリゴヌクレオチドを含む。更に2つのアンチセンスオリゴヌクレオチドは、同じアンチセンスオリゴヌクレオチドの複数のコピーの組み合わせ及び/または複数の異なるアンチセンスオリゴヌクレオチドの個々のコピーを含み得る。
特定の実施形態では、医薬組成物は、配列番号37~85からなる群から選択される配列を含むアンチセンスオリゴヌクレオチドを含む。いくつかの実施形態では、医薬組成物は、配列番号37~74からなる群から選択される配列を含むアンチセンスオリゴヌクレオチドを含む。いくつかの態様では、医薬組成物は、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含むアンチセンスオリゴヌクレオチドを含む。特定の態様では、医薬組成物は、配列番号52を含むアンチセンスオリゴヌクレオチドを含む。いくつかの実施形態では、医薬組成物は、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含むアンチセンスオリゴヌクレオチドを含む。特定の実施形態では、医薬組成物は、配列番号73を含むアンチセンスオリゴヌクレオチドを含む。
いくつかの実施形態では、医薬組成物は、潜在性エクソンをコードするSTMN2 mRNA配列に結合する有効量の薬剤(例えば、アンチセンスオリゴヌクレオチド)及び有効量の第2の薬剤を含む。いくつかの態様では、第2の薬剤は、神経変性障害を処置または阻害する薬剤である。いくつかの態様では、第2の薬剤は、外傷性脳損傷を処置または阻害する薬剤である。いくつかの態様では、第2の薬剤は、プロテアソーム阻害剤誘導性ニューロパチーを処置または阻害する薬剤である。
いくつかの実施形態では、医薬組成物は、不完全なまたは変化したSTMN2 RNA配列に結合する有効量の薬剤(例えば、アンチセンスオリゴヌクレオチド)及び有効量のSTMN2(例えば、遺伝子治療薬として投与される)を含む。
いくつかの実施形態では、医薬組成物は、不完全なまたは変化したSTMN2 RNA配列に結合する有効量の第1の薬剤(例えば、アンチセンスオリゴヌクレオチド)及びJNKを阻害する第2の薬剤を含む。
いくつかの実施形態では、医薬組成物は、潜在性エクソンをコードするSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に結合する有効量の薬剤(例えば、アンチセンスオリゴヌクレオチド)、有効量の第2の薬剤、及び薬学的に許容される担体、希釈剤、または賦形剤を含む。
不完全なまたは変化したSTMN2 RNA配列に結合する薬剤(例えば、アンチセンスオリゴヌクレオチド)を含む組成物は、TDP-43の機能の減退またはTDP病変に関連する疾患または状態を処置するために使用され得る。いくつかの態様では、不完全なまたは変化したSTMN2 RNA配列に結合する薬剤(例えば、アンチセンスオリゴヌクレオチド)を含む組成物は、本明細書に記載されている、(例えば、神経細胞における)STMN2タンパク質のレベルの変異または低減に関連する疾患または状態を処置するために使用され得る。
処置方法
本開示は、正常長STMN2 RNAまたはタンパク質をコードするSTMN2 RNAを回復させる薬剤(例えば、アンチセンスオリゴヌクレオチド)を含む組成物を利用する様々な処置方法を企図する。いくつかの態様では、薬剤(例えば、アンチセンスオリゴヌクレオチド)は、TDP-43の機能が減退しているかまたはTDP病変が存在する場合に発生しかつ存在量が増加するSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、それにより不完全なまたは変化したSTMN2 RNA配列の包含を抑制または防止する。いくつかの態様では、薬剤は、正常な完全長STMN2 RNAまたはタンパク質をコードするSTMN2 RNAの発現を回復させる。いくつかの態様では、薬剤は、STMN2 RNAへの潜在性エクソンの包含を抑制または防止する。いくつかの態様では、薬剤は、STMN2のタンパク質発現を活性化する。
本開示は、正常長STMN2 RNAまたはタンパク質をコードするSTMN2 RNAを回復させる薬剤(例えば、アンチセンスオリゴヌクレオチド)を含む組成物を利用する様々な処置方法を企図する。いくつかの態様では、薬剤(例えば、アンチセンスオリゴヌクレオチド)は、TDP-43の機能が減退しているかまたはTDP病変が存在する場合に発生しかつ存在量が増加するSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、それにより不完全なまたは変化したSTMN2 RNA配列の包含を抑制または防止する。いくつかの態様では、薬剤は、正常な完全長STMN2 RNAまたはタンパク質をコードするSTMN2 RNAの発現を回復させる。いくつかの態様では、薬剤は、STMN2 RNAへの潜在性エクソンの包含を抑制または防止する。いくつかの態様では、薬剤は、STMN2のタンパク質発現を活性化する。
いくつかの態様では、本開示は、疾患がTDP-43の機能の減退またはTDP病変に関連する、任意の疾患または状態の処置を企図する。いくつかの実施形態では、本明細書に開示される発明は、神経細胞におけるTDP-43のレベルの変異または低減(例えば、TDP-43関連病変を有する疾患または状態)を処置する方法に関する。いくつかの実施形態では、本明細書に開示される発明は、TDP-43関連認知症(例えば、ALS、FTD、アルツハイマー病、パーキンソン病、またはTBI)を処置する方法に関する。
いくつかの実施形態では、本明細書に開示される発明は、TDP-43のレベルの変異、増加、または低減に関連する疾患または状態を処置する方法に関する。いくつかの実施形態では、本明細書に開示される発明は、誤局在化したTDP-43に関連する疾患または状態を処置する方法に関する。いくつかの実施形態では、本明細書に開示される発明は、STMN2タンパク質のレベルの変異もしくは低減、及び/またはSTMN2タンパク質の誤局在化に関連する疾患または状態を処置する方法に関する。いくつかの実施形態では、本明細書に開示される発明は、プロテアソーム阻害剤誘導性ニューロパチー(例えば、機能的な核内TDP-43の量の低減の結果として生じるニューロパチー)に関連する疾患または状態を処置する方法に関する。いくつかの実施形態では、本明細書に開示される発明は、神経変性障害を処置する方法に関する。いくつかの実施形態では、本明細書に開示される発明は、TBI(例えば、脳震盪)に関連するか、またはその結果として生じる障害または状態を処置する方法に関する。
いくつかの態様では、TDP-43(例えば、核内TDP-43)のレベルの変異または低減は、STMN2タンパク質のレベルを変異させるかまたは低減させる。TDP-43の誤局在化は、サイトゾルにおけるTDP-43のレベルを増加させ得るが、核内TDP-43のレベルを低下させ得る。更に、STMN2レベルは、TDP-43の変異の結果として低下し得る。いくつかの態様では、TDP-43(例えば、核内TDP-43)のレベルの変異または増加は、STMN2タンパク質のレベルを変異させるかまたは低減させる。
いくつかの態様では、処置方法は、STMN2タンパク質のレベルの増加及び/またはSTMN2タンパク質の分解もしくは遅延の防止を含む。いくつかの態様では、処置方法は、STMN2タンパク質のレベルの変異または低減を補正することを含む。いくつかの態様では、処置方法は、STMN2 RNAの量または活性を増加させることを含む。いくつかの態様では、処置方法は、STMN2タンパク質の量を増加させること、例えば、タンパク質発現の活性化を増大させることを含む。いくつかの態様では、処置方法は、STMN2 RNA(例えば、STMN2 mRNA)への潜在性エクソンの包含を抑制または防止することを含む。いくつかの態様では、処置方法は、神経突起成長及び軸索再生をレスキューすることを含む。
いくつかの実施形態では、処置方法は、有効量の薬剤(例えば、アンチセンスオリゴヌクレオチド)を対象に投与することを含み、この薬剤は、STMN2タンパク質の分解を防止する。いくつかの実施形態では、処置方法は、有効量の薬剤を対象に投与することを含み、この薬剤は、正常長STMN2 RNAまたはタンパク質をコードするSTMN2 RNAを回復させる。いくつかの実施形態では、処置方法は、有効量の薬剤を対象に投与することを含み、この薬剤は、不完全なまたは変化したSTMN2 RNA配列に結合する。いくつかの実施形態では、処置方法は、有効量の薬剤を対象に投与することを含み、この薬剤は、(例えば、神経細胞における)STMN2 RNAへの潜在性エクソンの包含を抑制または防止する。いくつかの態様では、薬剤は、エクソンスキッピングを通じてSTMN2レベルを増加させる。いくつかの態様では、薬剤は、オリゴヌクレオチド、タンパク質、または小分子である。例えば、薬剤は、潜在性エクソンをコードするSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合するオリゴヌクレオチド(例えば、アンチセンスオリゴヌクレオチド)であり得る。
特定の実施形態では、処置方法は、有効量のアンチセンスオリゴヌクレオチドを対象に投与することを含み、このアンチセンスオリゴヌクレオチドは、配列番号37~85からなる群から選択される配列を含む。いくつかの態様では、処置方法は、有効量のアンチセンスオリゴヌクレオチドを対象に投与することを含み、このアンチセンスオリゴヌクレオチドは、配列番号37~74からなる群から選択される配列を含む。いくつかの実施形態では、処置方法は、有効量のアンチセンスオリゴヌクレオチドを対象に投与することを含み、このアンチセンスオリゴヌクレオチドは、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含む。いくつかの実施形態では、処置方法は、有効量のアンチセンスオリゴヌクレオチドを対象に投与することを含み、このアンチセンスオリゴヌクレオチドは、配列番号52を含む。いくつかの実施形態では、処置方法は、有効量のアンチセンスオリゴヌクレオチドを対象に投与することを含み、このアンチセンスオリゴヌクレオチドは、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含む。いくつかの実施形態では、処置方法は、有効量のアンチセンスオリゴヌクレオチドを対象に投与することを含み、このアンチセンスオリゴヌクレオチドは、配列番号73を含む。いくつかの実施形態では、神経変性疾患または障害(例えば、ALS、FTD、アルツハイマー病、パーキンソン病、またはTBI)を処置する方法は、配列番号37~85からなる群から、または代わりに配列番号37~74からなる群から選択される配列を含むアンチセンスオリゴヌクレオチドを対象に投与することを含む。いくつかの実施形態では、神経変性疾患または障害(例えば、ALS、FTD、アルツハイマー病、パーキンソン病、またはTBI)を処置する方法は、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含むアンチセンスオリゴヌクレオチドを対象に投与することを含む。いくつかの実施形態では、神経変性疾患または障害(例えば、ALS、FTD、アルツハイマー病、パーキンソン病、またはTBI)を処置する方法は、配列番号52を含むアンチセンスオリゴヌクレオチドを対象に投与することを含む。いくつかの実施形態では、神経変性疾患または障害(例えば、ALS、FTD、アルツハイマー病、パーキンソン病、またはTBI)を処置する方法は、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含むアンチセンスオリゴヌクレオチドを対象に投与することを含む。いくつかの実施形態では、神経変性疾患または障害(例えば、ALS、FTD、アルツハイマー病、パーキンソン病、またはTBI)を処置する方法は、配列番号73を含むアンチセンスオリゴヌクレオチドを対象に投与することを含む。いくつかの実施形態では、処置方法は、第2の薬剤を投与することを含む。
いくつかの実施形態では、薬剤(例えば、アンチセンスオリゴヌクレオチド)は、STMN2タンパク質レベルを増加及び/または回復させるために有効な量で(例えば、in vitroまたはin vivoで)投与される。
いくつかの態様では、薬剤(例えば、アンチセンスオリゴヌクレオチド)は、潜在性スプライシングを抑制する。いくつかの実施形態では、STMN2 RNAへの潜在性エクソンの包含を抑制または防止する薬剤で処置された対象は、ニューロン(例えば、運動性軸索)の成長及び/または修復の改善を示す。いくつかの態様では、薬剤は、STMN2タンパク質の分解を防止する。いくつかの態様では、薬剤は、運動失調、ニューロパチー、シナプス機能障害、認知の欠損、及び/または寿命の低下を含む神経変性疾患の症状を改善する。
いくつかの実施形態では、STMN2 RNAへの潜在性エクソンの包含は、ゲノム編集(例えば、CRISPR/Cas)を使用して抑制または防止される。
本明細書で使用される場合、「処置する(treat)」、「処置」、「処置する(treating)」、または「緩和」は疾患、障害または病態に関して使用される場合、状態の治療的処置を指し、その目的は、症状または状態の進行または重症度を逆転、軽減、緩和、阻害、減速または停止させることである。「処置する(treating)」という用語は、状態の少なくとも1つの有害な影響または症状を低減または軽減させることを含む。1つ以上の症状または臨床マーカーが低減した場合、処置は一般に「有効」である。あるいは、状態の進行が低減または停止した場合、処置は「有効」である。すなわち、「処置」には、症状またはマーカーの改善だけではなく、処置が行われない場合に予想される症状の進行または悪化を中断することまたは少なくとも減速させることも含まれる。有益なまたは望ましい臨床結果としては、1つ以上の症状(複数可)の軽減、欠損の程度の縮小、(例えば、神経変性障害の)安定化(すなわち、悪化しない)状態、神経変性障害の進行の遅延または減速、及び処置が行われない場合に予想されるものと比較した寿命の増加が挙げられるが、これらに限定されない。
「神経変性障害」は、神経幹細胞及び/または前駆細胞の変質のうちの少なくとも1つによって媒介されるか、または少なくとも部分的に特徴付けられる神経損失を含む疾患状態を指す。神経変性障害の非限定的な例としては、ポリグルタミン伸長障害(例えば、HD、歯状核赤核淡蒼球ルイ体萎縮症、ケネディ病(球脊髄性筋萎縮症とも称される)、及び脊髄小脳失調症(例えば、1型、2型、3型(マシャド・ジョセフ病とも称される)、6型、7型及び17型))、その他のトリヌクレオチドリピート伸長障害(例えば、脆弱性X症候群、脆弱性XE精神遅滞、フリードライヒ運動失調症、筋強直性ジストロフィー、脊髄小脳失調症8型、及び脊髄小脳失調症12型)、アレキサンダー病、アルパーズ病、アルツハイマー病、筋萎縮性側索硬化症(ALS)、毛細血管拡張性運動失調症、バッテン病(スピルマイヤー・フォークト・シェーグレン・バッテン病とも称される)、カナバン病、コケイン症候群、大脳皮質基底核変性症、クロイツフェルト・ヤコブ病、ギラン・バレー症候群、虚血性脳卒中、クラッベ病、クールー病、レビー小体型認知症、多発性硬化症、多系統萎縮症、非ハンチントン型舞踏病、パーキンソン病、ペリツェウス・メルツバッヘル病、ピック病、原発性側索硬化症、進行性核上性麻痺、レフサム病、サンドホフ病、シルダー病、脊髄損傷、脊髄筋萎縮症(SMA)、スティール・リチャードソン・オルゼウスキー病、前頭側頭型認知症(FTD)、ならびに脊髄癆が挙げられる。いくつかの状況において、神経変性障害は、身体的損傷(例えば、頭部外傷、軽度から重度の外傷性脳損傷(TBI)、びまん性軸索損傷、脳挫傷、急性脳腫脹など)に関連するCNSまたはPNSへの神経損傷またはダメージを包含する。
いくつかの実施形態では、神経変性障害は、神経細胞におけるTDP-43のレベルの変異または低減に関連する障害である。いくつかの実施形態では、神経変性障害は、STMN2タンパク質のレベルの変異もしくは低減、及び/またはSTMN2タンパク質の誤局在化に関連する障害である。いくつかの実施形態では、神経変性障害は、筋萎縮性側索硬化症(ALS)、前頭側頭型認知症(FTD)、前頭側頭葉変性症(FTLD)、アルツハイマー病、パーキンソン病、封入体筋炎(IBM)及びこれらの組み合わせからなる群から選択される。いくつかの態様では、神経変性障害は、ALSである。いくつかの態様では、神経変性障害は、FTD及び/またはFTLDと組み合わされたALSである。いくつかの態様では、神経変性障害は、アルツハイマー病である。いくつかの態様では、神経変性障害は、パーキンソン病である。
「プロテアソーム阻害剤誘導性ニューロパチー」は、本明細書では、機能的な核内TDP-43の量の低減の結果として生じる障害または状態を指すために使用される。核内TDP-43は、全体的なレベルで低下し得るか、またはレベルの低下は、核内TDP-43の排出を誘導するTDP-43の細胞質凝集の増加の結果として生じ得る。いくつかの態様では、プロテアソーム阻害は、STMN2の発現低下を招く。
「外傷性脳損傷」または「TBI」は、外力により脳が損傷したときに生じる頭蓋内損傷を指す。TBIは、その重症度(例えば、軽度、中等度、もしくは重度)、機序(例えば、閉鎖性もしくは穿通性頭部損傷)、またはその他の特徴(例えば、位置)に基づいて分類され得る。TBIは、身体症状、認知症状、社会症状、情緒症状、及び行動症状をもたらす可能性がある。TBIに関連する状態には、脳震盪が含まれる。TBI及びTBIに関連する状態は、TDP-43病変に関連している。いくつかの態様では、STMN2の変化は、TBIまたはそれに関連する状態において生じる。
いくつかの実施形態では、外傷性脳損傷は、神経細胞におけるTDP-43のレベルの変異に関連する障害であるか、またはそれをもたらす。いくつかの実施形態では、外傷性脳損傷は、STMN2タンパク質のレベルの変異もしくは低減、及び/またはSTMN2タンパク質の誤局在化に関連する障害であるか、またはそれをもたらす。いくつかの実施形態では、外傷性脳損傷の重症度は、神経細胞における機能的TDP-43の低下に基づいて測定される。いくつかの実施形態では、脳震盪の重症度は、神経細胞における機能的TDP-43の低下に基づいて測定される。
対象への投与のために、本明細書に開示される薬剤は、薬学的に許容される組成物で提供することができる。これらの薬学的に許容される組成物は、1つ以上の薬学的に許容される担体(添加剤)及び/または希釈剤とともに製剤化された、治療有効量の薬剤のうちの1つ以上を含む。本発明の医薬組成物は、固体または液体形態で投与するために特別に製剤化することができ、以下に適合するものを含む:(1)経口投与、例えば、水薬(水性もしくは非水性の溶液もしくは懸濁液)、胃管栄養、ロゼンジ、糖衣錠、カプセル剤、丸剤、錠剤(例えば、頬側、舌下、及び全身吸収を目的とするもの)、ボーラス、粉剤、顆粒剤、舌に適用するためのペースト;(2)非経口投与、例えば、滅菌溶液もしくは懸濁液、もしくは徐放性製剤としての、例えば、皮下注射、筋肉内注射、髄腔内注射、頭蓋骨間(intercranially)注射、静脈内注射もしくは硬膜外注射によるもの;(3)局所適用、例えば、皮膚に適用するクリーム、軟膏、もしくは制御放出パッチ、もしくはスプレーとして;(4)膣内もしくは直腸内、例えば、ペッサリー、クリームもしくは泡として;(5)舌下;(6)眼内;(7)経皮;(8)経粘膜;または(9)経鼻。更に、薬剤は患者に埋入することができ、または薬物送達システムを使用して注射することができる(例えば、Urquhart,et al.,Ann.Rev.Pharmacol.Toxicol.24:199-236(1984)、Lewis,ed.“Controlled Release of Pesticides and Pharmaceuticals”(Plenum Press,New York,1981)、米国特許第3,773,919号;及び同第35 3,270,960号を参照されたく、これらの全ての内容は参照により本明細書に組み込まれる)。
本明細書で使用される場合、「薬学的に許容される」という用語は、妥当な医学的判断の範囲内で、過度の毒性、刺激、アレルギー反応、またはその他の問題もしくは合併症を伴うことなく、ヒト及び動物の組織と接触させて使用するのに適しており、妥当な利益/リスク比に見合った薬剤、物質、組成物、及び/または剤形を指す。
本明細書で使用される場合、「薬学的に許容される担体」という用語は、1つの器官または身体の部分から、別の器官または身体の部分への対象薬剤の運搬または輸送に関与する、液体もしくは固体の充填剤、希釈剤、賦形剤、製造補助剤(例えば、滑沢剤、タルクマグネシウム、カルシウムもしくはステアリン酸亜鉛、もしくはステリック酸(steric acid))、または溶媒カプセル化物質などの、薬学的に許容される物質、組成物、またはビヒクルを意味する。各々の担体は、製剤の他の成分と適合し、かつ対象に有害ではないという意味において「許容され」なければならない。薬学的に許容される担体として機能し得る物質のいくつかの例としては、(1)ラクトース、グルコース、及びスクロースなどの糖類、(2)トウモロコシデンプン及びジャガイモデンプンなどのデンプン、(3)カルボキシメチルセルロースナトリウム、メチルセルロース、エチルセルロース、微結晶セルロース、及び酢酸セルロースなどのセルロースならびにその誘導体、(4)粉末トラガカント、(5)麦芽、(6)ゼラチン、(7)ステアリン酸マグネシウム、ラウリル硫酸ナトリウム、及びタルクなどの滑沢剤、(8)カカオバター及び坐剤用ワックスなどの賦形剤、(9)ピーナッツ油、綿実油、ベニバナ油、ゴマ油、オリーブ油、トウモロコシ油、及び大豆油などの油、(10)プロピレングリコールなどのグリコール、(11)グリセリン、ソルビトール、マンニトール、及びポリエチレングリコール(PEG)などのポリオール、(12)オレイン酸エチル及びラウリン酸エチルなどのエステル、(13)寒天、(14)水酸化マグネシウム及び水酸化アルミニウムなどの緩衝剤、(15)アルギン酸、(16)パイロジェンフリー水、(17)等張食塩水、(18)リンガー液、(19)エチルアルコール、(20)pH緩衝液、(21)ポリエステル、ポリカーボネート、及び/またはポリ無水物、(22)ポリペプチド及びアミノ酸などの増量剤、(23)血清アルブミン、HDL、及びLDLなどの血清成分、(22)エタノールなどのC2~C12アルコール、ならびに(23)医薬製剤に用いられる他の非毒性適合性物質が挙げられる。湿潤剤、着色剤、剥離剤、コーティング剤、甘味剤、香味剤、芳香剤、防腐剤、及び酸化防止剤も、製剤中に存在し得る。「賦形剤」、「担体」、「薬学的に許容される担体」などの用語は、本明細書において互換的に使用される。
本明細書で使用される場合、「治療有効量」という語句は、任意の医学的処置に適用可能な妥当な利益/リスク比で、動物の細胞の少なくとも亜集団において何らかの所望の治療効果を生じさせるのに有効である、本明細書に記載の薬剤を含む薬剤、物質、または組成物の量を意味する。例えば、対象に投与される薬剤の量は、統計学的に有意な、測定可能なTDP-43の機能の増加を生じさせるのに十分である。
本明細書に開示される薬剤及び組成物の治療有効量の決定は、十分に当業者の能力の範囲内である。一般に、治療有効量は、対象の既往、年齢、状態、性別、及び他の薬学的に活性な薬剤の投与によって変化し得る。
本明細書で使用される場合、「投与する」という用語は、所望の効果が生じるように、所望の部位における薬剤または組成物の少なくとも部分的な局在化をもたらす方法または経路による、対象(例えば、必要な対象)への薬剤または組成物の配置を指す。本発明の方法に適した投与経路には、局所及び全身の両方の投与経路が含まれる。一般に、局所投与は、対象の全身と比較して、投与された薬剤のより多くを特定の位置に送達させるのに対し、全身投与は、実質的に対象の全身へ薬剤を送達させる。
本明細書に開示される組成物及び薬剤は、静脈内投与、筋肉内投与、皮下投与、経皮投与、気道(エアロゾル)投与、経肺投与、経鼻投与、直腸投与、ならびに局所投与(頬側投与及び舌下投与を含む)を含む、経口または非経口経路を含むがこれらに限定されない、当該技術分野で公知の任意の適切な経路によって投与され得る。例示的な投与様式には、注射、注入、点滴注入、吸入、または摂取が含まれるが、これらに限定されない。「注射」には、限定されるわけではないが、静脈内、筋肉内、動脈内、髄腔内、脳室内、頭蓋内、嚢内、眼窩内、心臓内、皮内、腹腔内、経気管、皮下、表皮下、関節内、被膜下、くも膜下、脊髄内、脳脊髄内(intracerebro spinal)、及び胸骨内の注射及び注入が含まれる。本明細書に記載の態様の好ましい実施形態では、組成物は、静脈内注入または静脈内注射によって投与される。
本明細書で使用される場合、「対象」は、ヒトまたは動物(例えば、哺乳動物)を意味する。通常、動物は、霊長類、げっ歯類、家畜または狩猟動物などの脊椎動物である。霊長類には、チンパンジー、カニクイザル、クモザル、及びマカク(例えば、アカゲザル)が含まれる。家畜及び狩猟動物には、雌ウシ、ウマ、ブタ、シカ、バイソン、スイギュウ、ネコ種、例えば飼いネコ、イヌ種、例えばイヌ、キツネ、オオカミ、トリ種、例えばニワトリ、エミュー、ダチョウ、及び魚、例えばマス、ナマズ及びサケが含まれる。患者または対象には、前述の任意のサブセット、例えば、ヒト、霊長類またはげっ歯類などの1つ以上の群または種を除く上記の全てが含まれる。本明細書に記載の態様の特定の実施形態では、対象は哺乳動物、例えば、霊長類(例えば、ヒト)である。「患者」及び「対象」という用語は、本明細書では互換的に使用される。対象は、雄または雌であり得る。いくつかの実施形態では、対象は、(例えば、神経細胞における)TDP-43のレベルの変異または低減に関連する疾患または状態に罹患している。
スクリーニング方法
本開示は、TDP病変に関連する疾患もしくは状態を処置するか、またはその疾患もしくは状態の可能性を低減させるための候補薬剤を同定するための、1つ以上の試験薬剤(例えば、1つ以上のアンチセンスオリゴヌクレオチド)をスクリーニングする方法を企図する。いくつかの態様では、疾患または状態は、(例えば、神経細胞における)TDP-43のレベルの変異または低減に関連する。本開示は更に、STMN2タンパク質のレベルの変異または低減のいずれかに関連する疾患もしくは状態を処置するか、またはその疾患もしくは状態の可能性を低減させるための候補薬剤を同定するための、1つ以上の試験薬剤をスクリーニングする方法を企図する。
本開示は、TDP病変に関連する疾患もしくは状態を処置するか、またはその疾患もしくは状態の可能性を低減させるための候補薬剤を同定するための、1つ以上の試験薬剤(例えば、1つ以上のアンチセンスオリゴヌクレオチド)をスクリーニングする方法を企図する。いくつかの態様では、疾患または状態は、(例えば、神経細胞における)TDP-43のレベルの変異または低減に関連する。本開示は更に、STMN2タンパク質のレベルの変異または低減のいずれかに関連する疾患もしくは状態を処置するか、またはその疾患もしくは状態の可能性を低減させるための候補薬剤を同定するための、1つ以上の試験薬剤をスクリーニングする方法を企図する。
いくつかの実施形態では、本方法は、TDP-43レベルが低減した神経細胞を提供することと;この細胞を1つ以上の試験薬剤と接触させることと;接触させた細胞がSTMN2タンパク質のレベルの増加を有するか否かを判定することと;接触させた細胞がSTMN2タンパク質のレベルの増加を有する場合に、この試験薬剤を候補薬剤として同定することと、を含む。いくつかの態様では、接触させた細胞がSTMN2タンパク質のレベルの増加を有するか否かを判定するステップは、接触させた細胞中のSTMN2タンパク質レベルを測定することを含む。いくつかの態様では、STMN2タンパク質レベルは、ELISA(例えば、サンドイッチELISA)、ドットブロット、及び/またはウエスタンブロットを使用して測定される。いくつかの態様では、接触させた細胞がSTMN2タンパク質のレベルの増加を有するか否かを判定するステップは、接触させた細胞の形態または機能を評価することを含む。例えば、STMN2を欠くニューロンは、STMN2を有するニューロンの形態から変化した形態を有し得る。いくつかの態様では、接触させた細胞の形態または機能を、免疫ブロッティング及び/または免疫細胞化学を使用して評価する。いくつかの態様では、接触させた細胞を更に評価して、それが完全長STMN2 RNAを発現するか否かを判定することができる。STMN2 RNAの発現は、qRT-PCRを使用して測定することができる。
いくつかの実施形態では、本方法は、TDP-43レベルが変異した神経細胞を提供することと;この細胞を1つ以上の試験薬剤と接触させることと;接触させた細胞がSTMN2タンパク質のレベルの増加を有するか否かを判定することと;接触させた細胞がSTMN2タンパク質のレベルの増加を有する場合に、この試験薬剤を候補薬剤として同定することと、を含む。いくつかの態様では、接触させた細胞がSTMN2タンパク質のレベルの増加を有するか否かを判定するステップは、接触させた細胞中のSTMN2タンパク質レベルを測定することを含む。いくつかの態様では、STMN2タンパク質レベルは、ELISA、ドットブロット、及び/またはウエスタンブロットを使用して測定される。いくつかの態様では、接触させた細胞がSTMN2タンパク質のレベルの増加を有するか否かを判定するステップは、接触させた細胞の形態または機能を評価することを含む。例えば、STMN2を欠くか、またはSTMN2の量が低減しているニューロンは、正常レベルのSTMN2(すなわち、対照試料からのSTMN2のレベル)を有するニューロンの形態から変化した形態を有し得る。いくつかの態様では、接触させた細胞の形態または機能を、免疫ブロッティング及び/または免疫細胞化学を使用して評価する。いくつかの態様では、接触させた細胞を更に評価して、それが完全長STMN2 RNAを発現するか否かを判定することができる。STMN2 RNAの発現は、qRT-PCRを使用して測定することができる。
いくつかの実施形態では、本方法は、TDP-43レベルが低減した神経細胞を提供することと;この細胞を1つ以上の試験薬剤と接触させることと;接触させた細胞がSTMN2 RNA中に潜在性エクソンを有するか否かを判定することと、を含む。接触させた細胞をFISH RNA、またはRT-PCT、qPCR、qRT-PCR、またはRNAシーケンシングを使用して評価し、STMN2 RNA中に潜在性エクソンが存在するか否かを同定することができる。いくつかの実施形態では、本方法は、TDP-43レベルが低減した神経細胞を提供することと;この細胞を1つ以上の試験薬剤と接触させることと;接触させた細胞が完全長STMN2 RNAを発現するか否かを判定することと、を含む。接触させた細胞を、RNA FISHまたはRT-PCT、qPCR、qRT-PCR、またはRNAシーケンシングを使用して評価することができる。
いくつかの実施形態では、本方法は、TDP-43レベルが変異した神経細胞を提供することと;この細胞を1つ以上の試験薬剤と接触させることと;接触させた細胞がSTMN2 RNA中に潜在性エクソンを有するか否かを判定することと、を含む。接触させた細胞をFISH RNA、またはRT-PCT、qPCR、またはRNAシーケンシングを使用して評価し、STMN2 RNA中に潜在性エクソンが存在するか否かを同定することができる。いくつかの実施形態では、本方法は、TDP-43レベルが変異した神経細胞を提供することと;この細胞を1つ以上の試験薬剤と接触させることと;接触させた細胞が完全長STMN2 RNAを発現するか否かを判定することと、を含む。接触させた細胞を、RNA FISHまたはRT-PCT、qPCR、qRT-PCR、またはRNAシーケンシングを使用して評価することができる。
バイオマーカー
いくつかの態様では、本開示は、TDP-43の機能性の減退に関連する疾患または状態(例えば、実質的なTDP-43関連病変を有する疾患または状態)のためにSTMN2及び/またはELAVL3をバイオマーカーとして使用することを企図する。いくつかの態様では、STMN2及び/またはELAVL3は、疾患または状態の存在に関するバイオマーカーとして機能し得る。他の態様では、STMN2及び/またはELAVL3は、疾患または状態の進行をモニタリングするためのバイオマーカーとして機能し得る。いくつかの態様では、STMN2及び/またはELAVL3タンパク質レベルが評価される。いくつかの態様では、STMN2及び/またはELAVL3転写物レベルが評価される。
いくつかの態様では、本開示は、TDP-43の機能性の減退に関連する疾患または状態(例えば、実質的なTDP-43関連病変を有する疾患または状態)のためにSTMN2及び/またはELAVL3をバイオマーカーとして使用することを企図する。いくつかの態様では、STMN2及び/またはELAVL3は、疾患または状態の存在に関するバイオマーカーとして機能し得る。他の態様では、STMN2及び/またはELAVL3は、疾患または状態の進行をモニタリングするためのバイオマーカーとして機能し得る。いくつかの態様では、STMN2及び/またはELAVL3タンパク質レベルが評価される。いくつかの態様では、STMN2及び/またはELAVL3転写物レベルが評価される。
いくつかの実施形態では、疾患または状態は、神経細胞におけるTDP-43のレベルの変異または低減に関連する。いくつかの実施形態では、疾患または状態は、神経細胞におけるTDP-43のレベルの変異または増加に関連する。いくつかの実施形態では、疾患または状態は、神経変性疾患(例えば、筋萎縮性側索硬化症(ALS)、アルツハイマー病、パーキンソン病、または前頭側頭型認知症(FTD))である。いくつかの実施形態では、疾患または状態は、外傷性脳損傷に関連するか、またはその結果として生じる。
いくつかの態様では、TDP-43の機能性の減退に関連する疾患または状態を検出するための方法は、対象から試料を得ることと、試料を評価して、それがSTMN2及び/またはELAVL3タンパク質のレベルの変異または低減のいずれかを示すか否かを判定することと、を含む。いくつかの実施形態では、STMN2及び/またはELAVL3タンパク質レベルは、免疫ブロット、免疫細胞化学、ドットブロット、及び/またはELISAを含む、当業者に公知の任意の方法を使用して測定される。特定の態様では、STMN2及び/またはELAVL3タンパク質レベルは、ELISAを使用して測定される。いくつかの態様では、TDP-43の機能性の減退に関連する疾患または状態を検出するための方法は、対象から試料を得ることと、試料を評価して、それがSTMN2及び/またはELAVL3転写物のレベルの低減を示すか否かを判定することと、を含む。いくつかの実施形態では、STMN2及び/またはELAVL3転写物レベルは、RNA FISH、RT-PCR、qPCR、またはRNAシーケンシングを含む、当業者に公知の任意の方法を使用して測定される。特定の態様では、STMN2及び/またはELAVL3転写物レベルは、qRT-PCRを使用して測定される。STMN2及び/またはELAVL3タンパク質及び/または転写物のレベルの低減は、疾患または障害の結果としてのTDP-43の機能性の減退に関する指標であり得る。いくつかの態様では、TDP-43の機能性の減退に関連する疾患または状態の進行は、(例えば、処置プロトコルに応じて)長時間にわたって対象からの複数の試料を分析し、STMN2及び/またはELAVL3タンパク質及び/または転写物のレベルをモニタリングすることにより評価される。
いくつかの態様では、対象における神経変性疾患(例えば、ALS、FTD、パーキンソン病、アルツハイマー病)を検出するための方法は、罹患対象から試料(例えば、生体液試料)を得ることと、試料がレベルの変化したSTMN2及び/またはELAVL3タンパク質を含有するか否かを判定することと、を含む。特定の態様では、判定は、ELISAを使用して行われる。いくつかの態様では、対象における神経変性疾患(例えば、ALS、FTD、パーキンソン病、アルツハイマー病)を検出するための方法は、罹患対象から試料(例えば、生体液試料)を得ることと、試料がレベルの低減したSTMN2及び/またはELAVL3転写物を含有するか否かを判定することと、を含む。試料のスクリーニングは、RNA FISH、RT-PCR、qPCR、またはRNAシーケンシングを使用して実施され得る。特定の態様では、STMN2及び/またはELAVL3転写物レベルは、qRT-PCRを使用して測定される。STMN2及び/またはELAVL3タンパク質及び/または転写物のレベルの低減は、神経変性疾患または障害の結果としてのTDP-43の機能性の減退に関する指標であり得る。
いくつかの態様では、対象における外傷性脳損傷(TBI)を検出するための方法は、対象から試料(例えば、生体液試料)を得ることと、試料がレベルの変化したSTMN2及び/またはELAVL3タンパク質を含有するか否かを判定することと、を含む。特定の態様では、判定は、ELISAを使用して行われる。いくつかの態様では、対象における外傷性脳損傷(TBI)を検出するための方法は、対象から試料(例えば、生体液試料)を得ることと、STMN2及び/またはELAVL3転写物のレベルの低減に関して試料をスクリーニングすることと、を含む。試料のスクリーニングは、RNA FISH、RT-PCR、qPCR、またはRNAシーケンシングを使用して実施され得る。特定の態様では、STMN2及び/またはELAVL3転写物レベルは、qRT-PCRを使用して測定される。STMN2及び/またはELAVL3タンパク質及び/または転写物のレベルの低減は、TBIの結果としてのTDP-43の機能性の減退に関する指標であり得る。
いくつかの態様では、本開示は、TDP-43の機能性の減退に関連する疾患または状態(例えば、実質的なTDP-43関連病変を有する疾患または状態)のためにSTMN2の潜在性バリアントをバイオマーカーとして使用することを企図する。いくつかの実施形態では、疾患または状態は、神経変性疾患(例えば、ALS、FTD、アルツハイマー病、パーキンソン病)である。いくつかの実施形態では、疾患または状態は、外傷性脳損傷に関連するか、またはその結果である。
いくつかの態様では、TDP-43の機能性の減退に関連する疾患または状態を検出するための方法は、対象から試料を得ることと、試料を評価して、それがSTMN2の潜在性バリアントを含むか否かを判定することと、を含む。いくつかの実施形態では、STMN2転写物は、RNA FISH、RT-PCR、qPCR、またはRNAシーケンシングを使用して評価される。特定の態様では、STMN2転写物は、qRT-PCRを使用して測定される。STMN2の潜在性バリアントの存在は、TDP-43の機能性の減退に関する指標であり得る。
いくつかの態様では、神経変性疾患を検出するための方法は、対象から試料(例えば、生体液試料)を得ることと、STMN2の潜在性バリアントに関して試料をスクリーニングすることと、を含む。試料のスクリーニングは、PCRを使用して実施され得る。STMN2の潜在性バリアントの存在は、神経変性疾患または障害の結果としてのTDP-43の機能性の減退に関する指標であり得る。
いくつかの態様では、TBIを検出するための方法は、対象から試料(例えば、生体液試料)を得ることと、STMN2の潜在性バリアントに関して試料をスクリーニングすることと、を含む。試料のスクリーニングは、PCRを使用して実施され得る。STMN2の潜在性バリアントの存在は、外傷性脳損傷の結果としてのTDP-43の機能性の減退に関する指標であり得る。
実施例1:
画期的な知見において、TDP-43(TAR DNA結合タンパク質43)は、ALSの多数の散発性症例及びFTDの多くのサブセットにおけるユビキチン陽性封入体の主要構成成分であることが見出された(7)。TDP-43は、主に核内DNA/RNA結合タンパク質(8)であり、転写調節(9)、スプライシング(10、11)、プレmiRNAプロセシング(12)、ストレス顆粒形成(13、14)、ならびにmRNAの輸送及び安定性(15、16)において機能的役割を有する。その後、常染色体優性であり明らかに原因となるTARDBPの変異がALS家系及びFTD家系の両方において同定され、遺伝学と神経変性に関する病理学とが結び付けられた(17~21)。したがって、散発性ALSと家族性ALSの両方を理解するためには、TDP-43の誤局在化及び変異が疾患において担う役割を解明することが不可欠である。
画期的な知見において、TDP-43(TAR DNA結合タンパク質43)は、ALSの多数の散発性症例及びFTDの多くのサブセットにおけるユビキチン陽性封入体の主要構成成分であることが見出された(7)。TDP-43は、主に核内DNA/RNA結合タンパク質(8)であり、転写調節(9)、スプライシング(10、11)、プレmiRNAプロセシング(12)、ストレス顆粒形成(13、14)、ならびにmRNAの輸送及び安定性(15、16)において機能的役割を有する。その後、常染色体優性であり明らかに原因となるTARDBPの変異がALS家系及びFTD家系の両方において同定され、遺伝学と神経変性に関する病理学とが結び付けられた(17~21)。したがって、散発性ALSと家族性ALSの両方を理解するためには、TDP-43の誤局在化及び変異が疾患において担う役割を解明することが不可欠である。
TDP-43病変に関連する神経変性が、機能喪失機序、毒性獲得機序、または両者の組み合わせのいずれの結果であるかは未だ不明である(22)。初期の研究では、野生型TDP-43と変異型TDP-43の両方の過剰発現が、その凝集及び核局在化の喪失につながることが示された(22)。これらの研究は、TARDBP変異の常染色体優性遺伝パターンとともに、毒性獲得の見解を支持するように思われるが、核内TDP-43の喪失(一般的にその凝集に関連する)により、その正常な機能もまた損なわれている可能性があることが示唆される。その後の知見から、発生中の胚または有糸分裂後の運動ニューロンにおけるTDP-43の枯渇が、重大な結果をもたらし得ることが明らかとなった(23~27)。
TDP-43がニューロンのRNA代謝において果たしている無数の役割を考慮すると、TDP-43の誤局在化の際に誤調節されるRNA基質は何か、そしてそれらはいかにして運動ニューロパチーの一因となっているのか、という重要な疑問が生じた。この疑問に答えるための初期の取り組みは、TARDBPノックダウンを受けた患者またはマウスのいずれかからの全脳ホモジネートのRNAシーケンシング(RNA-seq)による架橋及び免疫沈降を利用した(11、28)。これらの結果として得られた発見により、多くの転写物がUGリピートと長いイントロンとを含む長いRNAを優先してTDP-43によって調節されるという一般的な理解につながった。しかしながら、これらの実験でシーケンシングされた脳ホモジネートにおいてグリアRNAが顕著であることにより、TDP-43の特異的なニューロン標的への洞察が制限された。結果として、TDP-43標的RNAと運動ニューロン変性の機序との間の明確な関係をほとんど構築することができなかった。
誤調節された場合にニューロン変性の一因となる基質を同定するために、精製ヒト運動ニューロン中でTDP-43によって調節されるRNAの同定に努めた。生存ALS患者の脆弱な運動ニューロンは、単離及び実験的摂動用に本質的に入手が困難であることから、ヒト多能性幹細胞を運動ニューロン(hMN)に誘導して、in vitroでALS及び他の神経変性状態を試験するための指向性分化アプローチが開発されている(29~31)。ここでは、TDP-43ノックダウン後にhMNのRNA-seqを実施し、TDP-43の欠損によってその存在量が正または負に調節される転写物を同定した。合計で、正常なRNAレベルを維持するためにTDP-43を必要とする885個の転写物を同定した。任意数のこれらの標的の誤調節が運動ニューロンの変性にわずかな役割を担っている可能性があるが、STMN2をコードする運動ニューロン中で最も豊富な転写物のうちの1つは、TARDBPの減退に対して特に感受性が高かったが、FUSまたはC9ORF72活性に対しては感受性が高くなかったことが認められた。更に、変異型TDP-43を発現するhMN及びプロテアソームが薬理学的に阻害されたhMNにおいても、STMN2レベルが低下することが判明し、これにより、げっ歯類ニューロンにおいてTDP-43の細胞質蓄積及び凝集が誘導されることが示された(32)。更に、微小管安定性の既知の調節因子であるSTMN2が、正常ヒト運動ニューロンの成長及び修復に必要なタンパク質をコードすることが示された。重要なことに、TDP-43活性の喪失の結果としてのSTMN2機能の喪失は、その発現もまた、ALS患者の運動ニューロンにおいて再現性よく低下していることが判明したことから、ALSを有する人々と機能的に関連している可能性がある。
結果
ヒト運動ニューロン(hMN)の分化及び精製
hMNを産生させるために、ヒト胚性幹細胞株HUES3 Hb9::GFP(33、34)を、改変14日方策を使用して接着培養条件(35、36)下でGFP+ hMNに分化させた(図7A)。このアプローチは、SMADシグナル伝達の小分子阻害を介した神経誘導、FGF及びNOTCHシグナル伝達阻害を介した神経分化の加速、ならびにレチノイン酸(RA)及びソニックヘッジホッグシグナル伝達経路の活性化を介したMNパターニングに依拠する(図7A)。分化14日目に、約18~20%のGFP+細胞を含む培養物を通常通り得た(図7B)。蛍光活性化細胞選別(FACS)の2日後に、得られた細胞の95%超が転写因子HB9を発現した(図7C~7D)。更に8日後、培養物は、転写因子Islet-1(80%)、ならびに汎ニューロン細胞骨格タンパク質β-IIIチューブリン(97%)及び微小管関連タンパク質2(MAP2)(90%)を発現するニューロンで構成されていた(図7E~7F)。FACS及び神経栄養因子を補充したグリア馴化培地での10日間の培養後の全細胞パッチクランプ記録により、これらの精製hMNが電気生理学的に活性であることが明らかとなった(図7G~7I)。脱分極の際に、hMNは、初期の速い内向き電流、続いて遅い外向き電流を示し、これは、機能的な電圧活性化ナトリウム及びカリウムチャネルの発現とそれぞれ一致した(図7G)。更に、hMNは反復活動電位を発火し(図7H)、興奮性神経伝達物質であるカイニン酸に応答した(図7I)。総合すると、これらのデータにより、これらの精製hMN培養物が期待される機能特性を有していることが実証された。
ヒト運動ニューロン(hMN)の分化及び精製
hMNを産生させるために、ヒト胚性幹細胞株HUES3 Hb9::GFP(33、34)を、改変14日方策を使用して接着培養条件(35、36)下でGFP+ hMNに分化させた(図7A)。このアプローチは、SMADシグナル伝達の小分子阻害を介した神経誘導、FGF及びNOTCHシグナル伝達阻害を介した神経分化の加速、ならびにレチノイン酸(RA)及びソニックヘッジホッグシグナル伝達経路の活性化を介したMNパターニングに依拠する(図7A)。分化14日目に、約18~20%のGFP+細胞を含む培養物を通常通り得た(図7B)。蛍光活性化細胞選別(FACS)の2日後に、得られた細胞の95%超が転写因子HB9を発現した(図7C~7D)。更に8日後、培養物は、転写因子Islet-1(80%)、ならびに汎ニューロン細胞骨格タンパク質β-IIIチューブリン(97%)及び微小管関連タンパク質2(MAP2)(90%)を発現するニューロンで構成されていた(図7E~7F)。FACS及び神経栄養因子を補充したグリア馴化培地での10日間の培養後の全細胞パッチクランプ記録により、これらの精製hMNが電気生理学的に活性であることが明らかとなった(図7G~7I)。脱分極の際に、hMNは、初期の速い内向き電流、続いて遅い外向き電流を示し、これは、機能的な電圧活性化ナトリウム及びカリウムチャネルの発現とそれぞれ一致した(図7G)。更に、hMNは反復活動電位を発火し(図7H)、興奮性神経伝達物質であるカイニン酸に応答した(図7I)。総合すると、これらのデータにより、これらの精製hMN培養物が期待される機能特性を有していることが実証された。
TDP-43のレベルが低減したhMNのRNA-Seq
ALSで観察される核内TDP-43の低減は、下流の神経変性事象に寄与し得る考えられる細胞機構として明らかになりつつある(7、37)。したがって、ノックダウンとRNA-Seqアプローチとの組み合わせにより、精製hMN集団においてTDP-43によって調節される特異的RNAを同定することが望まれた。Alexa Fluor 555にコンジュゲートした短鎖干渉RNAを使用して、まず、hMNへの高レベルの(約94.6%)siRNA送達を達成するためのトランスフェクション条件を検証した(図8A~8C)。次いで、TDP-43転写物を標的とする2つの別個のsiRNA(siTDP43)、いかなる特定の遺伝子も標的としないスクランブル配列を有する2つの対照siRNA(siSCR及びsiSCR_555)を使用して、siRNA送達後の異なる3つの時点(2日目、4日目及び6日目)において、精製hMN中でTDP-43 RNAiを行った(図8A)。siRNAトランスフェクション後、全RNA及びタンパク質をニューロンから単離した。qRT-PCRアッセイにより、siTDP43で処置したMNについて全ての時点でTDP-43 mRNAレベルのダウンレギュレーションが確認されたが、スクランブル対照で処置したものでは確認されず、siRNAトランスフェクションの4日後に最大ノックダウンが生じた(図8D)。更に、TDP-43の枯渇はまた、免疫ブロットアッセイによってタンパク質レベルで確認され、siTDP43処置MNは、TDP-43レベルの54~65%の低減を示した(図8E)。
ALSで観察される核内TDP-43の低減は、下流の神経変性事象に寄与し得る考えられる細胞機構として明らかになりつつある(7、37)。したがって、ノックダウンとRNA-Seqアプローチとの組み合わせにより、精製hMN集団においてTDP-43によって調節される特異的RNAを同定することが望まれた。Alexa Fluor 555にコンジュゲートした短鎖干渉RNAを使用して、まず、hMNへの高レベルの(約94.6%)siRNA送達を達成するためのトランスフェクション条件を検証した(図8A~8C)。次いで、TDP-43転写物を標的とする2つの別個のsiRNA(siTDP43)、いかなる特定の遺伝子も標的としないスクランブル配列を有する2つの対照siRNA(siSCR及びsiSCR_555)を使用して、siRNA送達後の異なる3つの時点(2日目、4日目及び6日目)において、精製hMN中でTDP-43 RNAiを行った(図8A)。siRNAトランスフェクション後、全RNA及びタンパク質をニューロンから単離した。qRT-PCRアッセイにより、siTDP43で処置したMNについて全ての時点でTDP-43 mRNAレベルのダウンレギュレーションが確認されたが、スクランブル対照で処置したものでは確認されず、siRNAトランスフェクションの4日後に最大ノックダウンが生じた(図8D)。更に、TDP-43の枯渇はまた、免疫ブロットアッセイによってタンパク質レベルで確認され、siTDP43処置MNは、TDP-43レベルの54~65%の低減を示した(図8E)。
hMNにおけるTDP-43の部分的喪失に応答した遺伝子発現の全体的な変化を捕捉するために、RNA-SeqライブラリーをsiRNA処置細胞から調製した(図1A)。次世代シーケンシングの後、100万あたりの転写物数(TPM)としてアノテーションした各遺伝子の発現データを得た。最初の教師なし階層クラスタリングにより、MN産生のバッチに基づく転写効果が明らかとなった(実験1対実験2)(図9A)。続くRNA-Seq試料の主成分分析では、500個の最も差次的に発現した遺伝子に焦点を当て、次いで、siTDP-43処置(pc1)に基づいて試料を分離したところ、TDP-43レベルの低減が確実な転写差をもたらし、MN産生のバッチ(pc2)がそれに続いたことが示された(図1B)。TDP-43転写物に関するTPM値の検査により、その存在量がsiTDP43で処置したMNにおいてのみ有意に低減したことを確認した(図9B)。次いで、DESeq2バイオインフォマティクスツール一式(38)を使用して差次的遺伝子発現解析を実施し、5%の偽発見率(FDR)で、TDP-43ノックダウン後のhMNにおいて合計885個の統計学的に差次的に発現する遺伝子を同定した(図1C~1D)。これらの細胞において、TPM値は、スクランブル配列siRNA対照で処置したMNにおけるTPM値と比較して、392個の遺伝子で有意に高く(「アップレギュレートされた」)、493個の遺伝子で有意に低かった(「ダウンレギュレートされた」)(図1C~1D)。
哺乳動物のCNSにおける数百の遺伝子の全転写レベルを変化させる(11)ことに加えて、TDP-43のレベルの低減は、遺伝子スプライシングにも影響を及ぼし得る(11、39~42)。スプライシングバリアントの包括的解析には、従来、スプライシング感受性エクソンアレイを必要とする(11、39)が、RNA-Seqリードのアイソフォームデコンヴォルーションのための計算的アプローチの開発が急速に進化している(43~45)。バイオインフォマティクスアルゴリズム「Cuffdiff 2」を用いたデータの限定的な試験(45)は、実際に、2つの重要なアイソフォームスイッチング事象を伴う差次的スプライシングのための筆頭候補としてPOLDIP3遺伝子を検出することができ(図9C)、これは、これまでin vitro及びin vivoの両方でTDP-43の機能の欠損に関連付けられていた(42、46)。
TDP-43ノックダウン後に有意に誤調節されたと同定した885個の遺伝子のうち、候補サブセットを更なる検証のために選択した。まず、ニューロン発現が豊富な遺伝子(STMN2(47、48)、ELAVL3(49))、ならびに神経発生及び神経障害と関連のある遺伝子(RCAN1(50)、NAT8L(51))を考慮した。更に、「陽性対照」として適正な発現レベル(TPM≧5)及び高い倍率変化を有する遺伝子(SELPLG、NAT8L)を、これらの候補がより強力であり、かつ検証の見込みがあると仮定されていたため、考慮した。次に、TDP-43ノックダウン後の独立した生物学的反復試験からRNAを得て、TARDBPを含む11個の候補遺伝子の相対発現レベルをqRT-PCRによって判定した。注目すべきことに、これらの11個の遺伝子のうち9個の差次的遺伝子発現が、スクランブル対照で処置したものと比較して、いずれかのsiTDP-43で処置した細胞において確認された(図1E~1F)。これらの結果は、選択された遺伝子間の再現可能な発現差を示しており、RNA-Seq解析からの知見を確証する。
STMN2レベルは、変異型TDP-43を発現するhMNにおいてダウンレギュレートされる
次に、TDP-43枯渇後に存在量が変化したRNAのいずれかが、ALSの原因となるTDP-43の変異型の発現によっても摂動されるか否かが問われた。この目的のために、TARDBPに病原性変異を保有する患者iPS細胞由来の運動ニューロンにおいて、TDP-43ノックダウン後に再現性のよい発現の変化を示した推定TDP-43標的RNAを調査した(図10)。多能性幹細胞を用いたこれまでの経験に基づいて、指向性分化アプローチは、不均質な培養物を生じる傾向があり、定量的な比較解析を困難にすることが知られていた(52)。更に、有糸分裂前駆細胞の存在は、それらが培養物を圧倒し結果を歪める可能性があるため、特に問題となる。これらの障害を克服するために、細胞表面マーカーに対する242個の抗体を用いて、分化HUES3 Hb9::GFP細胞株に対して偏りのないFACSベースの免疫プロファイリング解析を実施し(53)、GFP+及びGFP細胞で濃縮されたシグネチャを同定した(図11A)。NCAM+/EpCAM-細胞を選別することにより、培養物から増殖中のEdu+細胞を除去し、多数の人工多能性幹細胞の分化にわたってMAP2+/Islet-1+ニューロンの数を正規化することができることが判明した(図11B~11D)。この細胞表面シグネチャを使用して、5つの対照iPSC株(11a、15b、17a、18a、及び20b)ならびに異なるTDP-43変異を有する4つのiPSC株(36a(Q343R)、47d(G298S)、CS(M337V)、及びRB20(A325T))を分化させ、得られたMNをFACS精製した。予想通り、各iPS細胞株は、NCAM+ MNに分化する独自の性向を示した(図11E~11F)。しかしながら、選別後、全てのiPSC株について均質なニューロン培養物が得られた(図2B)。
次に、TDP-43枯渇後に存在量が変化したRNAのいずれかが、ALSの原因となるTDP-43の変異型の発現によっても摂動されるか否かが問われた。この目的のために、TARDBPに病原性変異を保有する患者iPS細胞由来の運動ニューロンにおいて、TDP-43ノックダウン後に再現性のよい発現の変化を示した推定TDP-43標的RNAを調査した(図10)。多能性幹細胞を用いたこれまでの経験に基づいて、指向性分化アプローチは、不均質な培養物を生じる傾向があり、定量的な比較解析を困難にすることが知られていた(52)。更に、有糸分裂前駆細胞の存在は、それらが培養物を圧倒し結果を歪める可能性があるため、特に問題となる。これらの障害を克服するために、細胞表面マーカーに対する242個の抗体を用いて、分化HUES3 Hb9::GFP細胞株に対して偏りのないFACSベースの免疫プロファイリング解析を実施し(53)、GFP+及びGFP細胞で濃縮されたシグネチャを同定した(図11A)。NCAM+/EpCAM-細胞を選別することにより、培養物から増殖中のEdu+細胞を除去し、多数の人工多能性幹細胞の分化にわたってMAP2+/Islet-1+ニューロンの数を正規化することができることが判明した(図11B~11D)。この細胞表面シグネチャを使用して、5つの対照iPSC株(11a、15b、17a、18a、及び20b)ならびに異なるTDP-43変異を有する4つのiPSC株(36a(Q343R)、47d(G298S)、CS(M337V)、及びRB20(A325T))を分化させ、得られたMNをFACS精製した。予想通り、各iPS細胞株は、NCAM+ MNに分化する独自の性向を示した(図11E~11F)。しかしながら、選別後、全てのiPSC株について均質なニューロン培養物が得られた(図2B)。
更に10日間のニューロン培養後、これらのFACS精製MNからの全RNAを採取し、qRT-PCRを実施して、最も再現性よくTDP-43枯渇の影響を受けた遺伝子産物(ALOX5AP、STMN2、ELAVL3、及びRCAN1)のレベルを調査した。遺伝子のうちの2つ(STMN2及びELAVL3)について、転写物レベルの有意な低下が観察された(図2C~2F)。TDP-43枯渇実験と一致して、密接に関連するSTMN1 RNAの存在量に対する有意な変化は観察されず、TDP-43とSTMN2との間の特異的な関係が示唆された(図2H、図12E)。更に、変異ニューロンと対照ニューロンとの間のTDP-43転写物レベルの有意差は観察されなかった(図2G)。総合すると、これらのデータは、TDP-43における病原性点変異の存在は、それ自体のレベルに影響を及ぼすことなくSTMN2及びELAVL3のmRNAレベルを変化させることができることを意味する。
続いて、標的転写物を調節するTDP-43の能力をALS関連変異がいかにして妨げることができるのかを調査した。先行研究は、変異型TDP-43を発現するiPSC株に由来するhMNが、TDP-43病変のいくつかの側面(可溶性及び不溶性の両方の細胞タンパク質抽出物へのその蓄積(54、55)ならびに細胞質誤局在化(56)を含む)を再現することを報告している。変異ニューロンにおける核内TDP-43の低下は、siRNAによって誘導される部分的喪失に類似し得ることから、TDP-43誤局在化の徴候を免疫蛍光法を使用して試験した。しかし、対照ニューロン及び変異ニューロンの両方において、主にTDP-43の核染色が観察された(図2I)。ピアソンの相関係数分析によりこれらの観察結果が裏付けられ、変異ニューロン及び対照ニューロンの両方について、TDP-43免疫染色とDNA対比染色との間の強い相関が明らかとなった(図2J)。これらの結果は、一部のTDP-43 iPS疾患モデリング研究(56)と一致しているが、他の研究(54)とは一致しておらず、TDP-43誤局在化を誘導するためには更なる細胞摂動が必要であり得る可能性が生じた(57)。まとめると、データは、TDP-43枯渇後に影響を受けた遺伝子のサブセットが、変異型TDP-43を発現するニューロンにおいても変化しており、これらの変化がTDP-43の特徴的な細胞質凝集に先行することを示唆している。したがって、少なくともこれらの限られた数の転写物の視点から、データは、TDP-43の変異が機能喪失型の転写表現型に部分的に寄与し得ることを示唆している。
STMN2レベルはhMNにおいてTDP-43により調節される
変異型TDP-43を発現するニューロン及びTDP-43枯渇後の両方においてスタスミン様2(STMN2)の転写物の低下が見られたのは、興味深いことであった。STMN2は、ニューロン細胞骨格の調節及び軸索再生経路において機能的役割を有する微小管結合タンパク質のスタスミンファミリーに属する4つのタンパク質(STMN1、STMN2、SCLIP/STMN3,及びRB3/STMN4)のうちの1つである(47,48,58~62)。ヒトにおいては、STMN1及びSTMN3遺伝子は遍在的発現を示すが、STMN2及びSTMN4はCNS組織に濃縮されている(63)。ALSにおける細胞骨格経路の関連性(64~66)及びCNS内でのその濃縮に関するエビデンスの増加を考慮して、STMN2とTDP-43との関係を更に特徴付けることに焦点を当てることとした。
変異型TDP-43を発現するニューロン及びTDP-43枯渇後の両方においてスタスミン様2(STMN2)の転写物の低下が見られたのは、興味深いことであった。STMN2は、ニューロン細胞骨格の調節及び軸索再生経路において機能的役割を有する微小管結合タンパク質のスタスミンファミリーに属する4つのタンパク質(STMN1、STMN2、SCLIP/STMN3,及びRB3/STMN4)のうちの1つである(47,48,58~62)。ヒトにおいては、STMN1及びSTMN3遺伝子は遍在的発現を示すが、STMN2及びSTMN4はCNS組織に濃縮されている(63)。ALSにおける細胞骨格経路の関連性(64~66)及びCNS内でのその濃縮に関するエビデンスの増加を考慮して、STMN2とTDP-43との関係を更に特徴付けることに焦点を当てることとした。
まず、STMN2転写物の著しいダウンレギュレーションが、STMN2タンパク質のレベルも低減させるか否かを試験した。独立したRNAi実験において、STMN2 mRNAに結合する2つの異なるプライマー対のセットを用いてqRT-PCRを実施したところ、siTDP43処置hMNにおいて、対照と比較して有意なダウンレギュレーション(約50~60%)が認められた(図3A)。次いで、免疫ブロットアッセイをhMNタンパク質溶解物で行ったところ、STMN2タンパク質レベルもまた、siTDP-43で処置したhMNにおいて低減することが認められた(図3B)。
次に、他の2つのALS関連遺伝子であるFUSまたはC9ORF72(5、67)のダウンレギュレーションもまた、hMN中のSTMN2レベルを変化させるか否かを考察した。TDP-43と構造的に類似したFUSタンパク質もRNA代謝に関与しており(68)、FUSバリアントは家族性ALS及びFTDの症例で検出されている(69)。C9ORF72の機能は活発な研究領域であるが、C9ORF72のイントロン領域における大きなリピート伸長が、相当数の家族性及び散発性ALS及びFTD症例の原因となっている(70~72)。TDP-43、FUS、またはC9ORF72を標的とするRNAiの誘導後、qRT-PCRによるそれぞれのsiRNA標的遺伝子の有意なダウンレギュレーションが認められた。(図12A~12C)。TDP-43のダウンレギュレーションは、FUSまたはC9ORF72の発現レベルを変化させず、FUSまたはC9ORF72のいずれかの発現の低減は、他のALS関連遺伝子に対する影響を示さなかった(図12A~12C)。TDP-43のノックダウンは更にSTMN2のレベルを低減させたが、FUSまたはC9ORF72の場合は低減させなかった(図3C)。重要なことに、これらの結果は、STMN2のダウンレギュレーションがRNAi誘導の結果ではなく、TDP-43の部分的喪失に応答する特異的分子機構であることを実証する。
TDP-43は、高度に保存されたRNA認識モチーフ(73)を介してRNA分子に結合しそれらを調節することができる。TDP-43が多くの標準的なTDP-43結合モチーフを有するSTMN2 RNAと直接会合するか否かを判定するために(図12F~12G)、TDP-43免疫沈降のための条件を策定し(図3D)、続いてホルムアルデヒドRNA免疫沈降(fRIP)を実施した。架橋を逆転させた後、定量的qRT-PCRを実施して結合したRNA分子を検出した。TDP-43 RNA転写物からの増幅を模索したが、これはこの自己調節がSTMN2転写物と同様に、十分に確立されているからである(11)。いずれの場合も、TDP-43プルダウン後の濃縮が観察されたが、IgG対照については、または異なるALS関連タンパク質であるSOD-1がプルダウンされた場合は観察されなかった(図3E~3F)。総合すると、結果はTDP-43がSTMN2 mRNAと直接会合し、TDP-43レベルの低減がSTMN2レベルの低減をもたらすことを示している。
hMNにおけるSTMN2の機能
次に、hMNにおけるSTMN2の機能について調査した。まず、STMN2の発現を、MNを産生する分化プロセスにわたって試験した(図12D)。先行する発現研究(62、63、74)を裏付けるように、STMN2タンパク質は、幹細胞またはニューロン前駆細胞において検出できなかったことから、分化ニューロンにおいて選択的に発現することが認められた(図12D)。次いで、免疫細胞化学を使用してSTMN2の細胞内局在化を探索したところ、STMN2が、神経突起先端に存在する個々の細胞質斑点に局在しており、核周囲領域に特に濃縮されていることが認められた(図3G)。ゴルジ関連タンパク質GOLGIN97に対するヒト特異的抗体を使用して、この領域がゴルジ装置に相当することを確認し(図3H)、STMN2 N末端が小胞輸送及び膜結合のためのパルミトイル化の標的であるという予測を実証した(75)。STMN2はまた、神経突起伸長及び損傷時に、成長円錐において機能することが予測されている(47)。分化及び選別の直後にhMNを染色すると、微小管と、成長円錐を定義する成分であるF-アクチン束との間の界面で、STMN2の強い染色が観察された(図3I)。これらの知見は、成長円錐におけるSTMN2微小管ダイナミクスの役割を裏付ける。総合すると、データは、STMN2がALSの病因に関与する細胞骨格欠損及び軸索輸送経路の変化において機能し得ることを示している(76)。
次に、hMNにおけるSTMN2の機能について調査した。まず、STMN2の発現を、MNを産生する分化プロセスにわたって試験した(図12D)。先行する発現研究(62、63、74)を裏付けるように、STMN2タンパク質は、幹細胞またはニューロン前駆細胞において検出できなかったことから、分化ニューロンにおいて選択的に発現することが認められた(図12D)。次いで、免疫細胞化学を使用してSTMN2の細胞内局在化を探索したところ、STMN2が、神経突起先端に存在する個々の細胞質斑点に局在しており、核周囲領域に特に濃縮されていることが認められた(図3G)。ゴルジ関連タンパク質GOLGIN97に対するヒト特異的抗体を使用して、この領域がゴルジ装置に相当することを確認し(図3H)、STMN2 N末端が小胞輸送及び膜結合のためのパルミトイル化の標的であるという予測を実証した(75)。STMN2はまた、神経突起伸長及び損傷時に、成長円錐において機能することが予測されている(47)。分化及び選別の直後にhMNを染色すると、微小管と、成長円錐を定義する成分であるF-アクチン束との間の界面で、STMN2の強い染色が観察された(図3I)。これらの知見は、成長円錐におけるSTMN2微小管ダイナミクスの役割を裏付ける。総合すると、データは、STMN2がALSの病因に関与する細胞骨格欠損及び軸索輸送経路の変化において機能し得ることを示している(76)。
hMNにおけるSTMN2レベルの低下の細胞での結果を調査するために、STMN2ノックアウト幹細胞を作製した。具体的には、CRISPR/Cas9媒介性ゲノム編集戦略(図4A)を使用して、2つのhES細胞株(WA01及びHUES3 Hb9::GFP)中のヒトSTMN2遺伝子座に大きな欠失を生成した。STMN2遺伝子に18kbの欠失を保有するクローンを同定するための一次PCRスクリーニング(図4B)を行った後、分化hMNにおけるタンパク質ノックアウトを、免疫ブロッティング及び免疫細胞化学の両方によって確認した(図4C~4D)。予想通り、親STMN2+/+株と比較した場合、候補欠失クローンに由来するhMNは、STMN2染色の完全な欠如を示すことが認められた。
微小管の動的不安定性を促進することにより軸索成長を調節するSTMN2の報告された役割(77)を考慮して、STMN2-/-hMNにおける神経突起成長を特徴付ける表現型アッセイを行った。培養7日後、選別したhMNを固定し、β-III-チューブリンについて染色し、神経突起を標識した(図4E)。体細胞の中心から所与の間隔での交差の数を定量化するSholl解析(78)により、STMN2+/+と比較した、STMN2-/-株における神経突起伸長の有意な低減が明らかとなった(図4F~4G)。これとは別に、神経突起伸長を増加させることが示されているROCK阻害剤Y-27632の存在下でニューロンを培養した。神経突起成長における差異は、STMN+/+株の成長を増強するがSTMN-/-株の成長を増強しない分子を用いたこれらの実験において更により際立っており、これにより、このシグナル伝達カスケードにおけるSTMN2の役割が示唆された(図4H)。同様の結果がWA01細胞株で観察された(図13)。
次に、STMN2がニューロン成長においてのみならず、損傷後のニューロン修復においても機能するか否かが問われた。これらの仮説を試験するために、選別したhMNを、神経細胞体由来の軸索の独立した培養を可能にするマイクロ流体デバイスに播種した(79)(図4I)。デバイスの体細胞区画中で7日間培養した細胞は、軸索をマイクロチャネルを通して軸索チャンバーへと伸長した(図4J)。軸索が体細胞区画の細胞体を妨げることなく実質的に切断されるまで、軸索チャンバーの真空吸引及び再潅流を繰り返し実施した。次に、損傷後の軸索修復を評価するために、経時的にマイクロチャネルから神経突起の長さを測定した。分析により、測定した全ての時点で、STMN2+/+と比較したSTMN2-/-株における再成長の有意な低減が明らかとなった(図4K)。同様の結果がWA01細胞株で観察された(図13)。総合すると、これらのデータは、STMN2のレベルの低減が、hMNにおける神経突起の成長及び複雑性、ならびに軸索切断後の修復に対して測定可能な表現型の影響を与え得ることを示している。
プロテアソーム機能はTDP-43局在化及びSTMN2レベルを調節する
先行研究により、hMNにおけるプロテアソーム阻害が変異型SOD-1の蓄積を誘発し得ることが立証された(31)。したがって、散発性ALSの潜在的モデルとして、MG-132媒介性プロテアソーム阻害がhMNにおけるTDP-43局在化に影響を及ぼすか否かを試験した。まず、明らかな細胞毒性を誘導することなくプロテアソームを阻害することができる小分子処置の範囲及びタイミングを確立した(図14A~14D)。プロテアソーム活性を正常活性の10%未満に低下させる一晩の1μMの処置に、ニューロンが耐え得ることを確認した(図14E)。次に、パルス追跡実験を実施して、TDP-43局在化に対するプロテアソーム阻害の結果を確認した(図5A)。驚くべきことに、前述のようにピアソンの相関係数分析を使用したところ、核におけるTDP-43染色はMG-132の24時間の1μMパルスの後に大幅に減少することが観察された(図5B~5C)。注目すべきことに、ウォッシュアウト後、TDP-43染色は4日後に未曝露のニューロンと区別不能となることが認められた(図5B~5C)。したがって、hMNにおけるプロテアソーム阻害は、可逆的なTDP-43の誤局在化を誘導する。これらの知見は、プロテアソーム阻害が同様にTDP-43核染色の喪失を引き起こした一次皮質及び海馬ニューロンに関するストレス条件試験と類似している(32)。
先行研究により、hMNにおけるプロテアソーム阻害が変異型SOD-1の蓄積を誘発し得ることが立証された(31)。したがって、散発性ALSの潜在的モデルとして、MG-132媒介性プロテアソーム阻害がhMNにおけるTDP-43局在化に影響を及ぼすか否かを試験した。まず、明らかな細胞毒性を誘導することなくプロテアソームを阻害することができる小分子処置の範囲及びタイミングを確立した(図14A~14D)。プロテアソーム活性を正常活性の10%未満に低下させる一晩の1μMの処置に、ニューロンが耐え得ることを確認した(図14E)。次に、パルス追跡実験を実施して、TDP-43局在化に対するプロテアソーム阻害の結果を確認した(図5A)。驚くべきことに、前述のようにピアソンの相関係数分析を使用したところ、核におけるTDP-43染色はMG-132の24時間の1μMパルスの後に大幅に減少することが観察された(図5B~5C)。注目すべきことに、ウォッシュアウト後、TDP-43染色は4日後に未曝露のニューロンと区別不能となることが認められた(図5B~5C)。したがって、hMNにおけるプロテアソーム阻害は、可逆的なTDP-43の誤局在化を誘導する。これらの知見は、プロテアソーム阻害が同様にTDP-43核染色の喪失を引き起こした一次皮質及び海馬ニューロンに関するストレス条件試験と類似している(32)。
プロテアソーム阻害後にTDP-43に何が生じたかを確認するために、TDP-43レベルを、界面活性剤可溶性画分及び界面活性剤不溶性画分の両方で免疫ブロット分析によって試験した。低用量のMG-132で処置した対照ニューロンから得られた可溶性溶解物(図5A)では、TDP-43レベルの有意な低下が認められた(図5D)。UREA、すなわち不溶性画分を探索したところ、プロテアソーム阻害がTDP-43を不溶性となるように誘発することが見出された(図5D)。最後に、短期高用量または長期低用量のMG-132のいずれかで処置したニューロンにおけるSTMN2レベルを探索した。いずれの場合も、STMN2 mRNAレベルの有意な低下が観察された(図5E)。総合すると、これらのデータは、タンパク質恒常性をTDP-43局在化及びSTMN2レベルと結び付ける。
TDP-43はhMNにおける潜在性エクソンの出現を抑制する
TDP-43はRNAスプライシングを調節する核において重要な役割を果たしており、最近の研究は、非保存エクソンまたは潜在性エクソンを抑制してイントロンの完全性を維持するTDP-43の能力に光を当てている(80)。RNA転写物に潜在性エクソンが含まれている場合、多くの場合、それらの包含は、遺伝子産物の翻訳を妨害するか、またはナンセンス媒介性崩壊を促進することにより、遺伝子産物の正常レベルに影響を及ぼす可能性がある(80)。興味深いことに、TDP-43潜在性エクソンの抑制により調節される遺伝子の重複は、マウスとヒトの間で観察されていない(80)。ヒトがん細胞においてTDP-43によって再現性よく調節されることが観察された遺伝子における潜在性エクソンのエビデンスについて、シーケンシングデータを調査した(81)。これら95個の遺伝子のうち9個に、潜在性エクソンにマッピングされるリードが見出され、これらには、RNA-Seq実験で一貫してダウンレギュレートされたPFKPが含まれていた(図15A、図3C)。この観察に基づいて、TDP-43枯渇後のhMNにおいて一貫して誤調節されている他の遺伝子にマッピングされるRNA-Seqリードも精査した。ELAVL3及びSTMN2の両方における潜在性エクソンの包含に関する強力なエビデンスが見出された(図15B~15C)。次に、潜在性エクソンの包含が、プロテアソーム阻害後のhMNにおけるSTMN2レベルの低下の一因であり得るか否かが問われた。この目的を達成するために、潜在性エクソンを含有する転写物を検出するためのRT-PCRアッセイを開発した(図5F)。プロテアソーム阻害剤で処置されたhMNのみが、検出可能なレベルの予想されたPCR産物を有しており(図5G)、PCR産物のサンガーシーケンシングにより、予期されたスプライスジャンクションが確認された(図15D~15E)。データを総合すると、STMN2ダウンレギュレーションの機序は、TDP-43の枯渇及び誤局在化の両方に関して類似していることが示唆される。
TDP-43はRNAスプライシングを調節する核において重要な役割を果たしており、最近の研究は、非保存エクソンまたは潜在性エクソンを抑制してイントロンの完全性を維持するTDP-43の能力に光を当てている(80)。RNA転写物に潜在性エクソンが含まれている場合、多くの場合、それらの包含は、遺伝子産物の翻訳を妨害するか、またはナンセンス媒介性崩壊を促進することにより、遺伝子産物の正常レベルに影響を及ぼす可能性がある(80)。興味深いことに、TDP-43潜在性エクソンの抑制により調節される遺伝子の重複は、マウスとヒトの間で観察されていない(80)。ヒトがん細胞においてTDP-43によって再現性よく調節されることが観察された遺伝子における潜在性エクソンのエビデンスについて、シーケンシングデータを調査した(81)。これら95個の遺伝子のうち9個に、潜在性エクソンにマッピングされるリードが見出され、これらには、RNA-Seq実験で一貫してダウンレギュレートされたPFKPが含まれていた(図15A、図3C)。この観察に基づいて、TDP-43枯渇後のhMNにおいて一貫して誤調節されている他の遺伝子にマッピングされるRNA-Seqリードも精査した。ELAVL3及びSTMN2の両方における潜在性エクソンの包含に関する強力なエビデンスが見出された(図15B~15C)。次に、潜在性エクソンの包含が、プロテアソーム阻害後のhMNにおけるSTMN2レベルの低下の一因であり得るか否かが問われた。この目的を達成するために、潜在性エクソンを含有する転写物を検出するためのRT-PCRアッセイを開発した(図5F)。プロテアソーム阻害剤で処置されたhMNのみが、検出可能なレベルの予想されたPCR産物を有しており(図5G)、PCR産物のサンガーシーケンシングにより、予期されたスプライスジャンクションが確認された(図15D~15E)。データを総合すると、STMN2ダウンレギュレーションの機序は、TDP-43の枯渇及び誤局在化の両方に関して類似していることが示唆される。
STMN2はヒト成人一次脊髄MNで発現し、ALSにおいて変化する
最後に、in vitroでの知見がin vivoでのALS患者の運動ニューロンに関連するか否かを試験することを試みた。この目的のために、ヒト成人脊髄組織の免疫組織化学を使用して、対照及びALS患者におけるSTMN2発現を調査した。核内TDP-43染色の病理学的喪失及び細胞質TDP-43免疫反応性封入体の蓄積を典型的に示す散発性ALS症例由来の死後脊髄MNにおいて、STMN2タンパク質のレベルが変化することが予測された(7、37)。幹細胞由来のhMNで観察されたものと同様に、強力なSTMN2免疫反応性がヒト成人腰髄MNの細胞質領域に存在したが、周囲のグリア細胞には存在しなかった(図6A~6C)。対照症例3例(脊髄疾患のエビデンスなし)及びALS症例3例の腰髄組織切片において、強力なSTMN2免疫反応性を示すMNのパーセンテージを測定した。仮説と一致して、STMN2抗体に対する明らかな免疫反応性を有する腰髄MNのパーセンテージが、散発性ALS症例から採取した組織試料において有意に低減したことが認められた(図6D)。この結果は、ALS死後試料のいくつかの独立した発現試験によって更に裏付けられる。発現試験を実施するために、3つの試験でALS患者由来の運動ニューロンのレーザー切開が実施されてきた(82~84)。このデータを調査したところ、対照試料と比較してALS患者試料についてSTMN2転写物レベルの低下が観察された(図6E~6F)。
最後に、in vitroでの知見がin vivoでのALS患者の運動ニューロンに関連するか否かを試験することを試みた。この目的のために、ヒト成人脊髄組織の免疫組織化学を使用して、対照及びALS患者におけるSTMN2発現を調査した。核内TDP-43染色の病理学的喪失及び細胞質TDP-43免疫反応性封入体の蓄積を典型的に示す散発性ALS症例由来の死後脊髄MNにおいて、STMN2タンパク質のレベルが変化することが予測された(7、37)。幹細胞由来のhMNで観察されたものと同様に、強力なSTMN2免疫反応性がヒト成人腰髄MNの細胞質領域に存在したが、周囲のグリア細胞には存在しなかった(図6A~6C)。対照症例3例(脊髄疾患のエビデンスなし)及びALS症例3例の腰髄組織切片において、強力なSTMN2免疫反応性を示すMNのパーセンテージを測定した。仮説と一致して、STMN2抗体に対する明らかな免疫反応性を有する腰髄MNのパーセンテージが、散発性ALS症例から採取した組織試料において有意に低減したことが認められた(図6D)。この結果は、ALS死後試料のいくつかの独立した発現試験によって更に裏付けられる。発現試験を実施するために、3つの試験でALS患者由来の運動ニューロンのレーザー切開が実施されてきた(82~84)。このデータを調査したところ、対照試料と比較してALS患者試料についてSTMN2転写物レベルの低下が観察された(図6E~6F)。
考察
これらの試験から、数百の転写物の存在量は、ALS研究に関連してこれまで明らかにされてきたいくつかのRNAを含めて、ヒト運動ニューロンにおいてTDP-43によって調節されている可能性があることが示唆される。例えば、この知見はBDNF発現がTDP-43によって部分的に調節され得ることを示唆しており、このニューロトロフィンの発現低下がこれまでに観察されていること(85)を考慮すると、注目すべきである。MMP9は、SOD1 ALSマウスモデルにおいて、変性に対して最も感受性の高い運動ニューロンの集団を定義することがこれまでに示されている(86)。これらの試験により、TDP-43の機能の低減がこの因子の発現をより広範囲に誘導する可能性があり、このことが、変性に対する運動ニューロンの感度を高め得ることが示唆される。ここで同定された転写物の更なる調査により、TDP-43に対する摂動がいかにして運動ニューロン機能障害を招くかについての洞察がもたらされる可能性がある。
これらの試験から、数百の転写物の存在量は、ALS研究に関連してこれまで明らかにされてきたいくつかのRNAを含めて、ヒト運動ニューロンにおいてTDP-43によって調節されている可能性があることが示唆される。例えば、この知見はBDNF発現がTDP-43によって部分的に調節され得ることを示唆しており、このニューロトロフィンの発現低下がこれまでに観察されていること(85)を考慮すると、注目すべきである。MMP9は、SOD1 ALSマウスモデルにおいて、変性に対して最も感受性の高い運動ニューロンの集団を定義することがこれまでに示されている(86)。これらの試験により、TDP-43の機能の低減がこの因子の発現をより広範囲に誘導する可能性があり、このことが、変性に対する運動ニューロンの感度を高め得ることが示唆される。ここで同定された転写物の更なる調査により、TDP-43に対する摂動がいかにして運動ニューロン機能障害を招くかについての洞察がもたらされる可能性がある。
重要な未解決の疑問は、TDP-43の家族性変異の機構的意義とは何か、及びその影響が、TDP-43が散発性疾患患者において病理学的に再局在化したときに生じる事象とどのように関連しているのかということであった。TDP-43により調節される運動ニューロン転写物の同定により、家族性及び散発性疾患の両方に関連するTDP-43への異なる操作の潜在的影響を調査する機会が得られた。まず、TDP-43枯渇後に低減したと同定された標的RNAのサブセットが、TDP-43変異を有する患者から産生された運動ニューロンにおいて有意な発現変化を示すか否かが問われた。興味深いことに、RNA結合タンパク質ELAVL3及び微小管調節因子STMN2の発現には若干ではあるが有意な変化が認められたが、同定された他の推定標的では認められなかった。したがって、標的RNAの発現低減はTDP-43表現型であると考えられ、患者の変異は部分的な機能喪失型の影響を示した。
変異型TDP-43は、過剰発現すると凝集する傾向にあることがこれまでに示されている(22)。いくつかの研究においても、変異型TDP-43は、患者特異的運動ニューロンにおいて生来のレベルで発現した場合、同様に凝集する傾向にあることが示唆されている(54、56、57)。実験において、核内変異型TDP-43の凝集または喪失がSTMN2及びELAVL3の発現低下の一因となり得るか否かを判定するために、TDP-43をこれらの患者の運動ニューロンにおいて注意深くモニタリングしたが、そのような欠損は特定されなかった。検出範囲を下回る若干の核内TDP-43の喪失または不溶性がSTMN2及びELAVL3発現の観察された減退の原因であることは否定できないが、この知見は、特定の基質を処理するための変異タンパク質の親和性または能力が単に低減している可能性があるという考えと一致する。これらの潜在的仮説を識別するためには、本試験の範囲を超えた更なる生化学的実験が必要となる可能性がある。
家族性患者の運動ニューロンにおいて、変異型TDP-43のより大規模な凝集、または核内喪失が生じている場合、それは検出可能であると考えられる。プロテアソーム阻害が、TDP-43の劇的な核内喪失をその不溶性の蓄積とともに誘導することが認められた。プロテアソーム阻害がSOD1 ALS患者特異的幹細胞由来の運動ニューロンにおいて不溶性SOD1の蓄積をもたらすが、正常SOD1のみを保有する対照運動ニューロンにおいては蓄積をもたらさないことを発見した後に、この操作を実施するための着想が生じた(31)。興味深いことに、異なる状況において他者によって明らかに観察されたように(32)、プロテアソーム阻害は、疾患遺伝子型の制御下にあるか否かにかかわらず、核内TDP-43の喪失及びその不溶性の蓄積を引き起こした。この結果は、ALSが関与する任意数の変異または事象によって誘導されるプロテオスタシスの破壊が、散発性ALSにおける最も一般的な組織病理学的所見の上流にあり得ることを示唆していたことから、魅力的であった。この知見により、更に、TDP-43の細胞質への再局在化が、破壊されたプロテオスタシスに対する保護的かつ適応的な応答を最初にもたらす可能性があると考えられた(87)。しかし、この応答の生化学的性質及びこれらの複合体が受ける可能性のある液晶変換(liquid crystal conversion)が、一過性の応答を引き起こし、TDP-43によって調節される重要なRNAの運動ニューロンが慢性的に枯渇する病的状態になる可能性がある(88)。TDP-43標的がプロテアソーム阻害後に運動ニューロンから枯渇するという知見は、そのモデルと一致する。
数百のRNAがTDP-43の枯渇により影響を受けることが判明したが、全ての転写物がTDP-43の変化により等しく影響されるように思われるわけではなく、STMN2、ELAVL3をコードするものを含む若干数は、特に感受性が高いことが認められた。この観察結果は、患者におけるTDP-43病変の主要な影響、ならびにそれが運動ニューロパチー及び変性に果たす可能性のある役割は少数の標的RNAを介して伝播されるか、という実質的な治療上の意味を伴う重要な疑問を提起する。もしそうであれば、これらの重要なTDP-43標的の機能、それらが妨害される機序、及びそれらが回復され得るか否かを理解することは、運動ニューロンの機能性を回復させるためのTDP-43病変の下流の経路に注目を向けることができるため、重要であり得る。STMNオルソログの確立された機能及びSTMN2レベルに対するTDP-43枯渇の影響の大きさを考慮すると、それがそのような標的であり得るかどうかは疑問に思われた。
スタスミンファミリーのタンパク質は、微小管安定性の調節因子として認識されており、ハエの運動性軸索の生物学的性質を調節することが実証されている(77)。遺伝子編集を使用してSTMN2がヒト幹細胞由来運動ニューロンにおいて重要な機能を果たしているか否かを確認したところ、このタンパク質が欠如していると運動性軸索の成長及び修復の両方が著しく損なわれることが認められた。in vitroで産生されたhMNは、真正のMNと多くの分子的及び機能的特性を共有しているが(29)、ALSの幹細胞ベースモデルからの発見に関するin vivo検証は、疾患機序及び治療戦略とのそれらの関連性の重要な試験である(89)。したがって、ヒト成人脊髄組織を使用して、STMN2レベルがALSにおいて変化するという知見を立証するin vivoのエビデンスを提供した。STMN2の発現低減に関する考えられる機序は、潜在性エクソンの出現である。適切に標的化されたアンチセンスオリゴヌクレオチドは、このスプライシング事象を抑制し、STMN2の発現を回復させる可能性がある。
材料及び方法
細胞培養ならびにhESC及びhiPSCのMNへの分化
多能性幹細胞を、Matrigel(商標)(BD Biosciences)でコーティングした組織培養皿上でmTeSR1培地(Stem Cell Technologies)を用いて増殖させ、5%CO2インキュベーター内にて37℃で維持した。幹細胞を、1mM EDTA処置後に細胞の小凝集体として継代した。10μMのROCK阻害剤(Sigma、Y-27632)を、解離の16~24時間後に、細胞死を防止するために培養物に添加した。SMADシグナル伝達の二重阻害、NOTCH及びFGFシグナル伝達の阻害、ならびにレチノイン酸及びSHHシグナル伝達によるパターニングと組み合わせた、接着培養条件に基づく改変プロトコルを使用してMNを分化させた。簡潔に述べると、accutase(商標)(Stem Cell Technologies)を使用してES細胞を単一細胞に解離させ、ROCK阻害剤(10μM Y-27632、Sigma)を補充したmTeSR1培地(Stem Cell Technologies)を用いて、マトリゲルでコーティングした培養プレート上に80,000細胞/cm2の密度で播種した。細胞が100%の培養密度に達したとき、培地を、分化培地(1×B-27サプリメント(Gibco(登録商標))、1×N-2サプリメント(Gibco(登録商標))、1×Gibco(登録商標)GlutaMAX(商標)(Life Technologies(商標))及び100μM非必須アミノ酸(NEAA)を補充した、1/2 Neurobasal(Life Technologies(商標))1/2 DMEM-F12(Life Technologies(商標)))に交換した。この時点を、運動ニューロン分化の0日目(d0)と規定した。小分子による処置を以下の通り行った:d0~d5に、10μM SB431542(Custom Synthesis)、100nM LDN-193189(Custom Synthesis)、1μMレチノイン酸(Sigma)及び1μM Smoothendアゴニスト(Custom Synthesis);d6~d14に、5μM DAPT(Custom Synthesis)、4μM SU-5402(Custom Synthesis)、1μMレチノイン酸(Sigma)及び1μM Smoothendアゴニスト(Custom Synthesis)。
細胞培養ならびにhESC及びhiPSCのMNへの分化
多能性幹細胞を、Matrigel(商標)(BD Biosciences)でコーティングした組織培養皿上でmTeSR1培地(Stem Cell Technologies)を用いて増殖させ、5%CO2インキュベーター内にて37℃で維持した。幹細胞を、1mM EDTA処置後に細胞の小凝集体として継代した。10μMのROCK阻害剤(Sigma、Y-27632)を、解離の16~24時間後に、細胞死を防止するために培養物に添加した。SMADシグナル伝達の二重阻害、NOTCH及びFGFシグナル伝達の阻害、ならびにレチノイン酸及びSHHシグナル伝達によるパターニングと組み合わせた、接着培養条件に基づく改変プロトコルを使用してMNを分化させた。簡潔に述べると、accutase(商標)(Stem Cell Technologies)を使用してES細胞を単一細胞に解離させ、ROCK阻害剤(10μM Y-27632、Sigma)を補充したmTeSR1培地(Stem Cell Technologies)を用いて、マトリゲルでコーティングした培養プレート上に80,000細胞/cm2の密度で播種した。細胞が100%の培養密度に達したとき、培地を、分化培地(1×B-27サプリメント(Gibco(登録商標))、1×N-2サプリメント(Gibco(登録商標))、1×Gibco(登録商標)GlutaMAX(商標)(Life Technologies(商標))及び100μM非必須アミノ酸(NEAA)を補充した、1/2 Neurobasal(Life Technologies(商標))1/2 DMEM-F12(Life Technologies(商標)))に交換した。この時点を、運動ニューロン分化の0日目(d0)と規定した。小分子による処置を以下の通り行った:d0~d5に、10μM SB431542(Custom Synthesis)、100nM LDN-193189(Custom Synthesis)、1μMレチノイン酸(Sigma)及び1μM Smoothendアゴニスト(Custom Synthesis);d6~d14に、5μM DAPT(Custom Synthesis)、4μM SU-5402(Custom Synthesis)、1μMレチノイン酸(Sigma)及び1μM Smoothendアゴニスト(Custom Synthesis)。
GFP+MNの蛍光活性化細胞選別(FACS)
d14に、分化培養物を、5%CO2/37℃のインキュベーター内で1時間のaccutase(商標)処置を使用して単一細胞に解離させた。1000μLのPipetman(登録商標)を用いた穏やかなピペット操作を繰り返し(10~20回)用いて、単一細胞の調製を行った。細胞をスピンダウンし、PBSで1回洗浄し、選別緩衝液(pH7の1×カチオン不含PBS 15mM HEPES(Gibco(登録商標))、1% BSA(Gibco(登録商標))、1×ペニシリン-ストレプトマイシン(Gibco(登録商標))、1mM EDTA、及びDAPI(1μg/mL))に再懸濁させた。FACS分析及び精製の直前に、細胞を45μmフィルタに通した。BD FACS Aria IIセルソーターを通常通り使用して、Hb9::GFP+細胞を、10μM ROCK阻害剤(Sigma、Y-27632)ならびに10ng/mLの神経栄養因子GDNF、BDNF及びCNTF(R&D)を含むMN培地(Neurobasal(Life Technologies(商標))、1×N-2サプリメント(Gibco(登録商標))、B-27サプリメント(Gibco(登録商標))、GlutaMax及びNEAA)が入った採取チューブ内に精製した。DAPIシグナルを使用して細胞生存率を解明し、MNパターニング分子(RA及びSAG)に曝露されていない分化細胞を、緑色蛍光についてゲーティングするための陰性対照として使用した。Hb9::GFPレポーターを含有しない株については、単一細胞懸濁液を、NCAM(BD Bioscience、BDB557919、1:200)及びEpCAM(BD Bioscience、BDB347198、1:50)に対する抗体とともに選別緩衝液中で25分間インキュベートし、次いでPBS 1×で1回洗浄し、選別緩衝液中に再懸濁させた。RNA-Seq実験では、1ウェルあたり200,000個のGFP+細胞を、マトリゲルで予めコーティングした24ウェル組織培養皿に播種した。それぞれ10ng/mLのGDNF、BDNF及びCNTF(R&D Systems)を補充したMN培地を使用して、精製MNをフィーディングし、成熟させた。RNA-Seq実験及び最も下流のアッセイを、0.1mg/mlポリ-Dリジン(Invitrogen)及び5μg/mlラミニン(Sigma-Aldrich)でコーティングしたd10精製MN(FACS後10日間培養したもの)を増殖させたプレートで、おおよそ130000細胞/cm2の濃度で行った。
d14に、分化培養物を、5%CO2/37℃のインキュベーター内で1時間のaccutase(商標)処置を使用して単一細胞に解離させた。1000μLのPipetman(登録商標)を用いた穏やかなピペット操作を繰り返し(10~20回)用いて、単一細胞の調製を行った。細胞をスピンダウンし、PBSで1回洗浄し、選別緩衝液(pH7の1×カチオン不含PBS 15mM HEPES(Gibco(登録商標))、1% BSA(Gibco(登録商標))、1×ペニシリン-ストレプトマイシン(Gibco(登録商標))、1mM EDTA、及びDAPI(1μg/mL))に再懸濁させた。FACS分析及び精製の直前に、細胞を45μmフィルタに通した。BD FACS Aria IIセルソーターを通常通り使用して、Hb9::GFP+細胞を、10μM ROCK阻害剤(Sigma、Y-27632)ならびに10ng/mLの神経栄養因子GDNF、BDNF及びCNTF(R&D)を含むMN培地(Neurobasal(Life Technologies(商標))、1×N-2サプリメント(Gibco(登録商標))、B-27サプリメント(Gibco(登録商標))、GlutaMax及びNEAA)が入った採取チューブ内に精製した。DAPIシグナルを使用して細胞生存率を解明し、MNパターニング分子(RA及びSAG)に曝露されていない分化細胞を、緑色蛍光についてゲーティングするための陰性対照として使用した。Hb9::GFPレポーターを含有しない株については、単一細胞懸濁液を、NCAM(BD Bioscience、BDB557919、1:200)及びEpCAM(BD Bioscience、BDB347198、1:50)に対する抗体とともに選別緩衝液中で25分間インキュベートし、次いでPBS 1×で1回洗浄し、選別緩衝液中に再懸濁させた。RNA-Seq実験では、1ウェルあたり200,000個のGFP+細胞を、マトリゲルで予めコーティングした24ウェル組織培養皿に播種した。それぞれ10ng/mLのGDNF、BDNF及びCNTF(R&D Systems)を補充したMN培地を使用して、精製MNをフィーディングし、成熟させた。RNA-Seq実験及び最も下流のアッセイを、0.1mg/mlポリ-Dリジン(Invitrogen)及び5μg/mlラミニン(Sigma-Aldrich)でコーティングしたd10精製MN(FACS後10日間培養したもの)を増殖させたプレートで、おおよそ130000細胞/cm2の濃度で行った。
RNAi
精製GFP+ MNの培養物中のRNAiを、TDP-43 mRNAを標的とするSilencer(登録商標)Select siRNA(Life Technologies(商標))を用いて、またはあらゆるヒト転写物に結合することが予測されていないスクランブル配列を有する非標的化siRNA対照を用いて誘導した。凍結乾燥させたsiRNAをヌクレアーゼフリー水に再懸濁させ、使用できる状態になるまで20μMストックとして-20℃で保存した。トランスフェクションのために、製造業者の指示に従って、siRNAをOptimem(Gibco(登録商標))で希釈し、RNAiMAX(Invitrogen)と混合した。30分間のインキュベーション後、1:1のOptimem:MN培地(Neurobasal(Life Technologies(商標))、N2サプリメント(Gibco(登録商標))、B-27サプリメント(Gibco(登録商標))、GlutaMax及びNEAA)、ならびにそれぞれ10ng/mLのGDNF、BDNF及びCNTF(R&D)中で各ウェルの最終siRNA濃度が60nMとなるように、混合物をMN培養物に滴加した。トランスフェクションの12~16時間後、培地を交換した。RNA-Seq実験及び検証アッセイを、トランスフェクションの4日後に採取した材料を用いて行った。
精製GFP+ MNの培養物中のRNAiを、TDP-43 mRNAを標的とするSilencer(登録商標)Select siRNA(Life Technologies(商標))を用いて、またはあらゆるヒト転写物に結合することが予測されていないスクランブル配列を有する非標的化siRNA対照を用いて誘導した。凍結乾燥させたsiRNAをヌクレアーゼフリー水に再懸濁させ、使用できる状態になるまで20μMストックとして-20℃で保存した。トランスフェクションのために、製造業者の指示に従って、siRNAをOptimem(Gibco(登録商標))で希釈し、RNAiMAX(Invitrogen)と混合した。30分間のインキュベーション後、1:1のOptimem:MN培地(Neurobasal(Life Technologies(商標))、N2サプリメント(Gibco(登録商標))、B-27サプリメント(Gibco(登録商標))、GlutaMax及びNEAA)、ならびにそれぞれ10ng/mLのGDNF、BDNF及びCNTF(R&D)中で各ウェルの最終siRNA濃度が60nMとなるように、混合物をMN培養物に滴加した。トランスフェクションの12~16時間後、培地を交換した。RNA-Seq実験及び検証アッセイを、トランスフェクションの4日後に採取した材料を用いて行った。
免疫細胞化学
免疫蛍光法用に、細胞を氷冷4%PFAで15分間4℃で固定し、1×PBS中の0.2%Triton-Xで45分間透過処理し、1×PBS-T(0.1%Tween(登録商標)-20)中の10%ロバ血清で1時間ブロッキングした。次に、細胞を一次抗体(ブロッキング溶液で希釈)とともに4℃で一晩インキュベートした。1×PBS-Tで少なくとも4回の洗浄(それぞれ5分間のインキュベーション)を行った後、細胞を二次抗体と室温で1時間インキュベートした(ブロッキング溶液で希釈した)。核をDAPIで染色した。本試験では、以下の抗体を使用した:Hb9(1:100、DSHB、MNR281.5C10-c)、TUJ1(1:1000、Sigma、T2200)、MAP2(1:10000、Abcam ab5392)、Ki67(1:400、Abcam、ab833)、GFP(1:500、LifeTechnologies(商標)、A10262)、Islet1(1:500、Abcam ab20670)、TDP-43(1:500、ProteinTechGroup)、STMN2(1:4000、Novus)、AlexaFluor(商標)647-Phalloidin(1:200)。使用した二次抗体(488、555、594、及び647)は、AlexaFluor(商標)(1:1000、Life Technologies(商標))及びDyLight(1:500、Jackson ImmunoResearch Laboratories)であった。顕微鏡写真を、相関係数を決定するためにFIJIソフトウェアを使用して分析した。
免疫蛍光法用に、細胞を氷冷4%PFAで15分間4℃で固定し、1×PBS中の0.2%Triton-Xで45分間透過処理し、1×PBS-T(0.1%Tween(登録商標)-20)中の10%ロバ血清で1時間ブロッキングした。次に、細胞を一次抗体(ブロッキング溶液で希釈)とともに4℃で一晩インキュベートした。1×PBS-Tで少なくとも4回の洗浄(それぞれ5分間のインキュベーション)を行った後、細胞を二次抗体と室温で1時間インキュベートした(ブロッキング溶液で希釈した)。核をDAPIで染色した。本試験では、以下の抗体を使用した:Hb9(1:100、DSHB、MNR281.5C10-c)、TUJ1(1:1000、Sigma、T2200)、MAP2(1:10000、Abcam ab5392)、Ki67(1:400、Abcam、ab833)、GFP(1:500、LifeTechnologies(商標)、A10262)、Islet1(1:500、Abcam ab20670)、TDP-43(1:500、ProteinTechGroup)、STMN2(1:4000、Novus)、AlexaFluor(商標)647-Phalloidin(1:200)。使用した二次抗体(488、555、594、及び647)は、AlexaFluor(商標)(1:1000、Life Technologies(商標))及びDyLight(1:500、Jackson ImmunoResearch Laboratories)であった。顕微鏡写真を、相関係数を決定するためにFIJIソフトウェアを使用して分析した。
免疫ブロットアッセイ
TDP-43及びSTMN2タンパク質の発現レベルの分析用に、d10 MNを、プロテアーゼ・ホスファターゼ阻害剤(Roche)を含有するRIPA緩衝液(150mM塩化ナトリウム;1%Triton X-100;0.5%デオキシコール酸ナトリウム;0.1%SDS;50mM Tris pH8.0)中にて氷上で20分間溶解させ、高速で遠心分離した。24ウェル培養物のウェルあたり200μLのRIPA緩衝液を通常通り使用し、BCA(Thermo Scientific)による測定で約20μgである総タンパク質を得た。RIPA緩衝液で2回洗浄後、不溶性ペレットを200μlのUREA緩衝液(Bio-Rad)に再懸濁させた。免疫ブロットアッセイ用に、2~3μgの総タンパク質をSDS-PAGE(BioRad)によって分離し、PDVF膜(BioRad)に移し、TDP-43(1:1000、ProteinTech Group)、GAPDH(1:1000、Millipore)及びSTMN2(1:3000、Novus)に対する抗体でプローブした。不溶性ペレットを、対応するRIPA可溶性対応物のタンパク質濃度に基づいてロードした。同じPDVF膜を、Restore(商標)PLUS Western Blot Stripping Buffer(Thermo Scientific)を使用して2~3回免疫アッセイした。GAPDHレベルを使用して各試料を正規化し、LiCorソフトウェアを使用してタンパク質バンドシグナルを定量化した。
TDP-43及びSTMN2タンパク質の発現レベルの分析用に、d10 MNを、プロテアーゼ・ホスファターゼ阻害剤(Roche)を含有するRIPA緩衝液(150mM塩化ナトリウム;1%Triton X-100;0.5%デオキシコール酸ナトリウム;0.1%SDS;50mM Tris pH8.0)中にて氷上で20分間溶解させ、高速で遠心分離した。24ウェル培養物のウェルあたり200μLのRIPA緩衝液を通常通り使用し、BCA(Thermo Scientific)による測定で約20μgである総タンパク質を得た。RIPA緩衝液で2回洗浄後、不溶性ペレットを200μlのUREA緩衝液(Bio-Rad)に再懸濁させた。免疫ブロットアッセイ用に、2~3μgの総タンパク質をSDS-PAGE(BioRad)によって分離し、PDVF膜(BioRad)に移し、TDP-43(1:1000、ProteinTech Group)、GAPDH(1:1000、Millipore)及びSTMN2(1:3000、Novus)に対する抗体でプローブした。不溶性ペレットを、対応するRIPA可溶性対応物のタンパク質濃度に基づいてロードした。同じPDVF膜を、Restore(商標)PLUS Western Blot Stripping Buffer(Thermo Scientific)を使用して2~3回免疫アッセイした。GAPDHレベルを使用して各試料を正規化し、LiCorソフトウェアを使用してタンパク質バンドシグナルを定量化した。
RNA調製、qRT-PCR、及びRNAシーケンシング
RNA-seq実験及びTrizol LS(Invitrogen)を使用する検証アッセイ用に、製造業者の指示に従ってd10 MNから全RNAを単離した。24ウェル培養物のウェルあたり500μLを添加した。合計300~1000ngの全RNAを使用して、iSCRIPTキット(Bio-rad)に従って逆転写によりcDNAを合成した。次に、SYBRグリーン(Bio-Rad)及びiCyclerシステム(Bio-rad)を使用して定量RT-PCR(qRT-PCR)を実施した。アッセイした全ての遺伝子の定量レベルを、GAPDH発現を使用して正規化した。正規化した発現を、関連する対照試料(大部分がsired処置したMNまたは1×TDP-43レベルを有する細胞)に対して表示した。患者株間の比較のために、正規化した発現を、プールしたデータポイントの平均に対して表示した。全てのプライマー配列は、要請に応じて入手可能である。次世代RNAシーケンシング(RNA-Seq)では、siRNA試料あたり少なくとも2つの技術的複製物またはAAVS1-TDP43遺伝子型を分析に含めた。RNA抽出後、bioAnalyzerにより決定したRNA完全性数(RIN)が7.5超の試料を、ライブラリー調製に使用した。簡潔に述べると、製造業者の指示に従ってillumina TruSeq RNAキットv2を使用して、約250ngの全RNAからRNAシーケンシングライブラリーを作製した。ライブラリーを、Harvard Bauer Core Sequencing施設において、HiSeq2000プラットフォームでシーケンシングした。全てのFASTQファイルを、bcbioRNASeqワークフロー及びツールチェーンを使用して分析した(90)。FASTQファイルを、GRCh37/hg19参照ゲノムにアラインメントした。差次的発現試験を、DESeq2バイオインフォマティクスツール一式を使用して実施した(38)。CufflinksのCuffdiffモジュールを使用して、差次的スプライシングを同定した。Salmonを使用してカウントを生成し、tximportを使用して遺伝子レベルでそれらをロードした(91、92)。次いで、全てのp値を、BenjaminiとHochbergの方法(93)を使用して、多重比較用に補正する。
RNA-seq実験及びTrizol LS(Invitrogen)を使用する検証アッセイ用に、製造業者の指示に従ってd10 MNから全RNAを単離した。24ウェル培養物のウェルあたり500μLを添加した。合計300~1000ngの全RNAを使用して、iSCRIPTキット(Bio-rad)に従って逆転写によりcDNAを合成した。次に、SYBRグリーン(Bio-Rad)及びiCyclerシステム(Bio-rad)を使用して定量RT-PCR(qRT-PCR)を実施した。アッセイした全ての遺伝子の定量レベルを、GAPDH発現を使用して正規化した。正規化した発現を、関連する対照試料(大部分がsired処置したMNまたは1×TDP-43レベルを有する細胞)に対して表示した。患者株間の比較のために、正規化した発現を、プールしたデータポイントの平均に対して表示した。全てのプライマー配列は、要請に応じて入手可能である。次世代RNAシーケンシング(RNA-Seq)では、siRNA試料あたり少なくとも2つの技術的複製物またはAAVS1-TDP43遺伝子型を分析に含めた。RNA抽出後、bioAnalyzerにより決定したRNA完全性数(RIN)が7.5超の試料を、ライブラリー調製に使用した。簡潔に述べると、製造業者の指示に従ってillumina TruSeq RNAキットv2を使用して、約250ngの全RNAからRNAシーケンシングライブラリーを作製した。ライブラリーを、Harvard Bauer Core Sequencing施設において、HiSeq2000プラットフォームでシーケンシングした。全てのFASTQファイルを、bcbioRNASeqワークフロー及びツールチェーンを使用して分析した(90)。FASTQファイルを、GRCh37/hg19参照ゲノムにアラインメントした。差次的発現試験を、DESeq2バイオインフォマティクスツール一式を使用して実施した(38)。CufflinksのCuffdiffモジュールを使用して、差次的スプライシングを同定した。Salmonを使用してカウントを生成し、tximportを使用して遺伝子レベルでそれらをロードした(91、92)。次いで、全てのp値を、BenjaminiとHochbergの方法(93)を使用して、多重比較用に補正する。
電気生理学的記録
GFP+MNを、ポリ-D-リジン/ラミニンコーティングカバースリップ上に5,000細胞/cm2の密度で播種し、MN培地中で10日間培養し、マウスグリア細胞で2~3日間馴化させて、それぞれ10ng/mLのGDNF、BDNF及びCNTF(R&D Systems)を補充した。電気生理学的記録を以前に報告されたように(31、94)行った。簡潔に述べると、Multiclamp 700B(Molecular Devices)を使用して、室温(21~23℃)で全細胞電圧クランプまたは電流クランプ記録を行った。Digidata 1440A A/Dインターフェースでデータをデジタル化し、pCLAMP 10_ソフトウェア(Molecular Devices)を使用して記録した。データを20kHzでサンプリングし、2kHzでローパスフィルタ処理した。パッチピペットを、Sutter Instruments P-97プラー上でホウケイ酸ガラスキャピラリーから引き抜き、抵抗は2~4MWであった。ピペットキャパシタンスを、パラフィルムでシャンクを包むことによって低減させ、増幅回路を使用して補償した。直列抵抗は、通常は5~10MWであり、常に15MW未満であり、少なくとも80%補償された。P/4プロトコルを使用して直線リーク電流(linear leakage current)をデジタル的に差し引いた。-80mVの保持電位から-80mV~30mVの範囲の試験電位まで10mV刻みで増加させ電圧を誘発した。細胞内溶液はカリウムベースの溶液であり、グルコン酸K、135;MgCl2、2;KCl、6;HEPES、10;Mg ATP、5;0.5(KOHを用いてpH7.4)を含有していた。細胞外はナトリウムベースであり、NaCl、135;KCl、5;CaCl2、2;MgCl2、1;グルコース、10;HEPES、10(NaOHを用いてpH7.4)を含有していた。カイニン酸はSigmaから購入した。
GFP+MNを、ポリ-D-リジン/ラミニンコーティングカバースリップ上に5,000細胞/cm2の密度で播種し、MN培地中で10日間培養し、マウスグリア細胞で2~3日間馴化させて、それぞれ10ng/mLのGDNF、BDNF及びCNTF(R&D Systems)を補充した。電気生理学的記録を以前に報告されたように(31、94)行った。簡潔に述べると、Multiclamp 700B(Molecular Devices)を使用して、室温(21~23℃)で全細胞電圧クランプまたは電流クランプ記録を行った。Digidata 1440A A/Dインターフェースでデータをデジタル化し、pCLAMP 10_ソフトウェア(Molecular Devices)を使用して記録した。データを20kHzでサンプリングし、2kHzでローパスフィルタ処理した。パッチピペットを、Sutter Instruments P-97プラー上でホウケイ酸ガラスキャピラリーから引き抜き、抵抗は2~4MWであった。ピペットキャパシタンスを、パラフィルムでシャンクを包むことによって低減させ、増幅回路を使用して補償した。直列抵抗は、通常は5~10MWであり、常に15MW未満であり、少なくとも80%補償された。P/4プロトコルを使用して直線リーク電流(linear leakage current)をデジタル的に差し引いた。-80mVの保持電位から-80mV~30mVの範囲の試験電位まで10mV刻みで増加させ電圧を誘発した。細胞内溶液はカリウムベースの溶液であり、グルコン酸K、135;MgCl2、2;KCl、6;HEPES、10;Mg ATP、5;0.5(KOHを用いてpH7.4)を含有していた。細胞外はナトリウムベースであり、NaCl、135;KCl、5;CaCl2、2;MgCl2、1;グルコース、10;HEPES、10(NaOHを用いてpH7.4)を含有していた。カイニン酸はSigmaから購入した。
ホルムアルデヒドRNA免疫沈降
hMNの6ウェルプレートのうちの1ウェル(200万細胞)を架橋させ、MagnaRIPの説明書(Millipore)に従って処理した。本試験では、以下の抗体を使用した:SOD1(Cell Signaling Technologies)、TDP-43(FL9、D.Clevelandの寄贈品)、及びマウスIgG(cell signaling technology)。各RIP RNA画分のCt値を、RNA試料調製の差異を考慮して、同じqPCRアッセイのインプットRNA画分のCt値に対して正規化した。dCt[正規化RIP]を算出するために、Ct[RIP]-(Ct[インプット]-log2(インプット希釈係数))を決定し、希釈係数は100または1%であった。倍率濃縮を決定するために、dCt[正規化RIP]-dCt[正規化IgG]によるddCt、次いで倍率濃縮=2^-ddCtを算出した。
hMNの6ウェルプレートのうちの1ウェル(200万細胞)を架橋させ、MagnaRIPの説明書(Millipore)に従って処理した。本試験では、以下の抗体を使用した:SOD1(Cell Signaling Technologies)、TDP-43(FL9、D.Clevelandの寄贈品)、及びマウスIgG(cell signaling technology)。各RIP RNA画分のCt値を、RNA試料調製の差異を考慮して、同じqPCRアッセイのインプットRNA画分のCt値に対して正規化した。dCt[正規化RIP]を算出するために、Ct[RIP]-(Ct[インプット]-log2(インプット希釈係数))を決定し、希釈係数は100または1%であった。倍率濃縮を決定するために、dCt[正規化RIP]-dCt[正規化IgG]によるddCt、次いで倍率濃縮=2^-ddCtを算出した。
STMN2ノックアウトの作製
STMN2ガイドRNAを、以下のウェブリソース:Schier LabのCHOPCHOP(chopchop.rc.fas.harvard.edu)(95)を使用して設計した。ヒトU6プロモーターを含有するベクター(Broad Institute,Cambridgeのカスタム合成)にガイドをクローニングし、続いて、BbsIによる切断及びアンピシリン耐性によって利用可能なクローニング部位にクローニングした。クローニングを実施するために、指図する前に全てのgRNAを修飾した。BbsI付着末端に適合するオーバーハングを生成するために、センス鎖の5’ヌクレオチドがGでない場合、このヌクレオチドを除去してGで置換;逆相補鎖の場合、最も3’側のヌクレオチドを除去してCで置換し、一方で5’末端にAAACを付加、という修飾を使用した。得られた修飾STMN2 gRNA配列をCas9ヌクレアーゼゲノム編集(ガイド1:5’CACCGTATAGATGTTGATGTTGCG3’(エクソン2)(配列番号4)、ガイド2:5’CACCTGAAACAATTGGCAGAGAAG3’(エクソン3)(配列番号5)、ガイド3:5’CACCAGTCCTTCAGAAGGCTTTGG3’(エクソン4)(配列番号6))に使用した。クローニングを、最初にPCRチューブ中の両方のgRNAをアニーリング及びリン酸化することにより実施した。濃度100μMの両方の鎖1μLを、1μLのT4 PNK(New England Biolabs)、1μLのT4ライゲーション緩衝液、及び6μLのH2Oに添加した。チューブをサーモサイクラーに入れ、37℃で30分間、続いて95℃で5分間インキュベートし、5℃/分の速度で25℃までゆっくりと下降させた。続いて、アニーリングしたオリゴを1:100に希釈し、2μLの100μM pUC6ベクター、2μLのNEB緩衝液2.1、1μLの10mM DTT、1μLの10mM ATP、1μLのBbsI(New England Biolabs)、0.5μLのT7リガーゼ(New England Biolabs)及び10.5μLのH2Oを含有するライゲーション反応物に2μLを添加した。この溶液を、37℃で5分間、続いて21℃で5分間のサイクルを合計6回繰り返してサーモサイクラー内でインキュベートした。続いて、ベクターをOneShot Top10(ThermoFisher Scientific)細胞にクローニングし、LB-アンピシリン寒天プレートに播種し、37℃で一晩インキュベートした。Qiagen MIDIprepキット(Qiagen)を使用してベクターを単離し、ナノドロップを使用してDNA濃度を測定した。M13F(-21)プライマーを使用してGenewizによってベクターをシーケンシングすることにより、適切なクローニングを確認した。
STMN2ガイドRNAを、以下のウェブリソース:Schier LabのCHOPCHOP(chopchop.rc.fas.harvard.edu)(95)を使用して設計した。ヒトU6プロモーターを含有するベクター(Broad Institute,Cambridgeのカスタム合成)にガイドをクローニングし、続いて、BbsIによる切断及びアンピシリン耐性によって利用可能なクローニング部位にクローニングした。クローニングを実施するために、指図する前に全てのgRNAを修飾した。BbsI付着末端に適合するオーバーハングを生成するために、センス鎖の5’ヌクレオチドがGでない場合、このヌクレオチドを除去してGで置換;逆相補鎖の場合、最も3’側のヌクレオチドを除去してCで置換し、一方で5’末端にAAACを付加、という修飾を使用した。得られた修飾STMN2 gRNA配列をCas9ヌクレアーゼゲノム編集(ガイド1:5’CACCGTATAGATGTTGATGTTGCG3’(エクソン2)(配列番号4)、ガイド2:5’CACCTGAAACAATTGGCAGAGAAG3’(エクソン3)(配列番号5)、ガイド3:5’CACCAGTCCTTCAGAAGGCTTTGG3’(エクソン4)(配列番号6))に使用した。クローニングを、最初にPCRチューブ中の両方のgRNAをアニーリング及びリン酸化することにより実施した。濃度100μMの両方の鎖1μLを、1μLのT4 PNK(New England Biolabs)、1μLのT4ライゲーション緩衝液、及び6μLのH2Oに添加した。チューブをサーモサイクラーに入れ、37℃で30分間、続いて95℃で5分間インキュベートし、5℃/分の速度で25℃までゆっくりと下降させた。続いて、アニーリングしたオリゴを1:100に希釈し、2μLの100μM pUC6ベクター、2μLのNEB緩衝液2.1、1μLの10mM DTT、1μLの10mM ATP、1μLのBbsI(New England Biolabs)、0.5μLのT7リガーゼ(New England Biolabs)及び10.5μLのH2Oを含有するライゲーション反応物に2μLを添加した。この溶液を、37℃で5分間、続いて21℃で5分間のサイクルを合計6回繰り返してサーモサイクラー内でインキュベートした。続いて、ベクターをOneShot Top10(ThermoFisher Scientific)細胞にクローニングし、LB-アンピシリン寒天プレートに播種し、37℃で一晩インキュベートした。Qiagen MIDIprepキット(Qiagen)を使用してベクターを単離し、ナノドロップを使用してDNA濃度を測定した。M13F(-21)プライマーを使用してGenewizによってベクターをシーケンシングすることにより、適切なクローニングを確認した。
幹細胞トランスフェクションを、100μLキット(ThermoFisher Scientific)を備えたNeon Transfection System(ThermoFisher Scientific)を使用して実施した。トランスフェクションの前に、幹細胞を10μMのRock阻害剤を含有するmTeSR1中で1時間インキュベートした。続いて、accutaseを添加し、37℃で5分間インキュベートすることにより、細胞を解離させた。細胞をCountessを使用して計数し、2.5×106細胞/mLの濃度でR培地に再懸濁させた。次いで、細胞溶液を、ガイドを含有する各ベクター1μgと、pSpCas9n(BB)-2A-Puro(PX462)V2.0(Feng Zhang(Addgene)からの寄贈品)1.5μgとを含有するチューブに添加した。ピューロマイシン耐性ベクターでトランスフェクトした場合、エレクトロポレーションした細胞を、10cm皿中の10μMのRock阻害剤を含有するプレインキュベートした37℃のmTeSR培地中に直ちに放出した。ピューロマイシン耐性ベクターによるトランスフェクションの24時間後、選択を開始した。培地を吸引し、異なる濃度のピューロマイシン(1μg/μL、2μg/μL、及び4μg/μL)を含有するmTESR1培地に交換した。更に24時間後、培地を吸引し、mTeSR1培地に交換した。細胞を10日間培養した後、コロニーを採取して細胞を24ウェルプレートに入れ、増殖させた。
Qiagen DNeasy Blood and Tissueキット(Qiagen)を使用してピューロマイシンで選択したコロニーからゲノムDNAを抽出し、PCRスクリーニングして、STMN2遺伝子中の目的の欠失の存在を確認した。PCR産物を、1%アガロースゲルでの電気泳動後に分析した。簡潔に述べると、標的配列を、欠失クローンを検出するために1100bpの欠失バンドを生成するように設計した、欠失の外部にある一対のプライマーによってPCR増幅した。使用したプライマーの配列は以下の通りである:OUT_FWD、5’GCAAAGGAGTCTACCTGGCA3’(配列番号7)及びOUT_REV、5’GGAAGGGTGACTGACTGCTC3’(配列番号8)。ノックアウト株を、免疫ブロット分析を使用して更に確認した。
神経突起成長アッセイ
Sholl解析に使用する個々のTuj1陽性ニューロンをランダムに選択し、40倍の対物レンズを備えたNikon Eclipse TE300を使用して画像化した。ImageJ(NIH)プラグインNeuronJ(78)を使用して神経突起を追跡し、FijiのShollツール(96)を使用してSholl解析を実施し、細胞体から10μm間隔での交差の数を定量化した。Prism6(Graph Pad,La Jolla,CA,USA)を使用して、各10μm間隔につきKOクローンと親WT株との交差の数を比較することにより、統計分析を実施した。有意性を標準的なスチューデントのt検定によって評価し、p<0.05のp値を有意であると見なした。
Sholl解析に使用する個々のTuj1陽性ニューロンをランダムに選択し、40倍の対物レンズを備えたNikon Eclipse TE300を使用して画像化した。ImageJ(NIH)プラグインNeuronJ(78)を使用して神経突起を追跡し、FijiのShollツール(96)を使用してSholl解析を実施し、細胞体から10μm間隔での交差の数を定量化した。Prism6(Graph Pad,La Jolla,CA,USA)を使用して、各10μm間隔につきKOクローンと親WT株との交差の数を比較することにより、統計分析を実施した。有意性を標準的なスチューデントのt検定によって評価し、p<0.05のp値を有意であると見なした。
軸索切断
選別した運動ニューロンを、0.1mg/mlポリ-D-リジン(Sigma-Aldrich)及び5μg/mlラミニン(Invitrogen)でコーティングしたガラスカバースリップ上にマウントした標準的なニューロンマイクロ流体デバイス(SND150、XONA Microfluidics)中で、おおよそ250,000ニューロン/デバイスの濃度で培養した。培養7日目に、軸索が体細胞区画の細胞体を妨げることなく実質的に切断されるまで、軸索チャンバーの真空吸引及び再潅流を繰り返すことにより軸索切断を実施した。
選別した運動ニューロンを、0.1mg/mlポリ-D-リジン(Sigma-Aldrich)及び5μg/mlラミニン(Invitrogen)でコーティングしたガラスカバースリップ上にマウントした標準的なニューロンマイクロ流体デバイス(SND150、XONA Microfluidics)中で、おおよそ250,000ニューロン/デバイスの濃度で培養した。培養7日目に、軸索が体細胞区画の細胞体を妨げることなく実質的に切断されるまで、軸索チャンバーの真空吸引及び再潅流を繰り返すことにより軸索切断を実施した。
TDP-43及びSTMN2の免疫組織化学的分析
Partners及びHarvard IRBプロトコルに準拠して、散発性ALS症例3例及び対照(脊髄疾患のエビデンスなし)3例の死後試料を、Massachusetts Alzheimer’s Disease Research Center(ADRC)から収集した。TDP-43免疫反応性(ウサギポリクローナル、ProteinTech Group)の組織学的分析を実施して、診断を確定した。STMN2分析では、ホルマリン固定腰髄切片を、ブロッキング前にクエン酸緩衝液抗原回復を実施したことを除いて、標準的な免疫組織化学的手順を使用して染色した。簡潔に述べると、試料を再水和させ、水ですすぎ、3%過酸化水素、次いで正常血清中でブロッキングし、一次STMN2ウサギ由来抗体(1:100希釈、Novus)とインキュベートし、続いて適切な二次抗体(西洋ワサビペルオキシダーゼにコンジュゲートした抗ウサギIgG、1:200)とインキュベートして、ABC Vectastainキット及びDABペルオキシダーゼ基質に曝露させ、ヘマトキシリンで短時間対比染色してからマウントした。各試料について複数のレベルを試験した。
Partners及びHarvard IRBプロトコルに準拠して、散発性ALS症例3例及び対照(脊髄疾患のエビデンスなし)3例の死後試料を、Massachusetts Alzheimer’s Disease Research Center(ADRC)から収集した。TDP-43免疫反応性(ウサギポリクローナル、ProteinTech Group)の組織学的分析を実施して、診断を確定した。STMN2分析では、ホルマリン固定腰髄切片を、ブロッキング前にクエン酸緩衝液抗原回復を実施したことを除いて、標準的な免疫組織化学的手順を使用して染色した。簡潔に述べると、試料を再水和させ、水ですすぎ、3%過酸化水素、次いで正常血清中でブロッキングし、一次STMN2ウサギ由来抗体(1:100希釈、Novus)とインキュベートし、続いて適切な二次抗体(西洋ワサビペルオキシダーゼにコンジュゲートした抗ウサギIgG、1:200)とインキュベートして、ABC Vectastainキット及びDABペルオキシダーゼ基質に曝露させ、ヘマトキシリンで短時間対比染色してからマウントした。各試料について複数のレベルを試験した。
STMN2スプライシング解析
RNeasy Mini Kit(Qiagen)を製造業者の指示に従って使用して、ニューロンから全RNAを単離した。合計300~1000ngの全RNAを使用して、iSCRIPTキット(Bio-rad)に従って逆転写によりcDNAを合成した。次に、1つの潜在性エクソン特異的プライマーを使用してRT-PCRを実施し、次いで、Agilent 2200 Tapestationを使用して解析した。
RNeasy Mini Kit(Qiagen)を製造業者の指示に従って使用して、ニューロンから全RNAを単離した。合計300~1000ngの全RNAを使用して、iSCRIPTキット(Bio-rad)に従って逆転写によりcDNAを合成した。次に、1つの潜在性エクソン特異的プライマーを使用してRT-PCRを実施し、次いで、Agilent 2200 Tapestationを使用して解析した。
統計分析
qRT-PCRアッセイ及びSTMN2免疫組織化学的分析の統計学的有意性を、対応のない両側スチューデントのt検定を使用して評価し、*p<0.05のp値を有意であると見なした。第二種の過誤は、慣習的なレベルである0.05で制御した。
qRT-PCRアッセイ及びSTMN2免疫組織化学的分析の統計学的有意性を、対応のない両側スチューデントのt検定を使用して評価し、*p<0.05のp値を有意であると見なした。第二種の過誤は、慣習的なレベルである0.05で制御した。
参照文献
1.Pasinelli,P.& Brown,R.H.Molecular biology of amyotrophic lateral sclerosis:insights from genetics.Nat.Rev.Neurosci.7,710-723(2006).
2.Rowland,L.P.& Shneider,N.A.Amyotrophic lateral sclerosis.New England Journal of Medicine 344,1688-1700(2001).
3.Ravits,J.et al.Deciphering amyotrophic lateral sclerosis:What phenotype,neuropathology and genetics are telling us about pathogenesis.Amyotroph Lateral Scler Frontotemporal Degener 14,5-18(2013).
4.Miller,R.G.,Mitchell,J.D.& Moore,D.H.Riluzole for amyotrophic lateral sclerosis(ALS)/motor neuron disease(MND).Cochrane Database Syst Rev 3,CD001447(2012).
5.Ling,S.-C.,Polymenidou,M.& Cleveland,D.W.Converging mechanisms in ALS and FTD:disrupted RNA and protein homeostasis.Neuron 79,416-438(2013).
6.Dion,P.A.,Daoud,H.& Rouleau,G.A.Genetics of motor neuron disorders:new insights into pathogenic mechanisms.Nat.Rev.Genet.10,769-782(2009).
7.Neumann,M.et al.Ubiquitinated TDP-43 in frontotemporal lobar degeneration and amyotrophic lateral sclerosis.Science 314,130-133(2006).
8.Chen-Plotkin,A.S.,Lee,V.M.-Y.& Trojanowski,J.Q.TAR DNA-binding protein 43 in neurodegenerative disease.Nature Reviews Neurology 6,211-220(2010).
9.Ignatius,S.H.,Wu,F.,Harrich,D.,GarciaMartinez,L.F.& Gaynor,R.B.Cloning and Characterization of a Novel Cellular Protein,Tdp-43,That Binds to Human-Immunodeficiency-Virus Type-1 Tar Dna-Sequence Motifs.J Virol 69,3584-3596(1995).
10.Buratti,E.et al.Nuclear factor TDP-43 and SR proteins promote in vitro and in vivo CFTR exon 9 skipping.EMBO J 20,1774-1784(2001).
11.Polymenidou,M.et al.Long pre-mRNA depletion and RNA missplicing contribute to neuronal vulnerability from loss of TDP-43.Nat Neurosci 14,459-468(2011).
12.Kawahara,Y.& Mieda-Sato,A.TDP-43 promotes microRNA biogenesis as a component of the Drosha and Dicer complexes.P Natl Acad Sci Usa 109,3347-3352(2012).
13.Liu-Yesucevitz,L.et al.Tar DNA Binding Protein-43(TDP-43)Associates with Stress Granules:Analysis of Cultured Cells and Pathological Brain Tissue.PLoS ONE 5,(2010).
14.Parker,S.J.et al.Endogenous TDP-43 localized to stress granules can subsequently form protein aggregates.Neurochem.Int.60,415-424(2012).
15.Alami,N.H.et al.Axonal transport of TDP-43 mRNA granules is impaired by ALS-causing mutations.Neuron 81,536-543(2014).
16.Volkening,K.,Leystra-Lantz,C.,Yang,W.,Jaffee,H.& Strong,M.J.Tar DNA binding protein of 43 kDa(TDP-43),14-3-3 proteins and copper/zinc superoxide dismutase(SOD1)interact to modulate NFL mRNA stability.Implications for altered RNA processing in amyotrophic lateral sclerosis(ALS).Brain Research 1305,168-182(2009).
17.Benajiba,L.et al.TARDBP mutations in motoneuron disease with frontotemporal lobar degeneration.Ann Neurol.65,470-473(2009).
18.Rutherford,N.J.et al.Novel Mutations in TARDBP(TDP-43)in Patients with Familial Amyotrophic Lateral Sclerosis.PLoS Genet 4,(2008).
19.Sreedharan,J.et al.TDP-43 mutations in familial and sporadic amyotrophic lateral sclerosis.Science 319,1668-1672(2008).
20.Van Deerlin,V.M.et al.TARDBP mutations in amyotrophic lateral sclerosis with TDP-43 neuropathology:a genetic and histopathological analysis.The Lancet Neurology 7,409-416(2008).
21.Yokoseki,A.et al.TDP-43 mutation in familial amyotrophic lateral sclerosis.Ann Neurol.63,538-542(2008).
22.Lee,E.B.,Lee,V.M.-Y.& Trojanowski,J.Q.Gains or losses:molecular mechanisms of TDP43-mediated neurodegeneration.Nat.Rev.Neurosci.13,38-50(2012).
23.Kraemer,B.C.et al.Loss of murine TDP-43 disrupts motor function and plays an essential role in embryogenesis.Acta Neuropathol 119,409-419(2010).
24.Sephton,C.F.et al.TDP-43 is a developmentally regulated protein essential for early embryonic development.J.Biol.Chem.285,6826-6834(2010).
25.Wu, L.-S., Cheng, W.-C.& Shen, C.-K.J.Targeted depletion of TDP-43 expression in the spinal cord motor neurons leads to the development of amyotrophic lateral sclerosis-like phenotypes in mice.J.Biol.Chem.287,27335-27344(2012).
26.Yang,C.et al.Partial loss of TDP-43 function causes phenotypes of amyotrophic lateral sclerosis.Proc.Natl.Acad.Sci.U.S.A.111,E1121-9(2014).
27.Iguchi,Y.et al.Loss of TDP-43 causes age-dependent progressive motor neuron degeneration.Brain 136,1371-1382(2013).
28.Tollervey,J.R.et al.Characterizing the RNA targets and position-dependent splicing regulation by TDP-43.Nat Neurosci 14,452-458(2011).
29.Davis-Dusenbery,B.N.,Williams,L.A.,Klim,J.R.& Eggan,K.How to make spinal motor neurons.Development 141,491-501(2014).
30.Han, S.S.W., Williams, L.A.& Eggan, K.C.Constructing and deconstructing stem cell models of neurological disease.Neuron 70,626-644(2011).
31.Kiskinis,E.et al.Pathways disrupted in human ALS motor neurons identified through genetic correction of mutant SOD1.Cell Stem Cell 14,781-795(2014).
32.van Eersel,J.et al.Cytoplasmic accumulation and aggregation of TDP-43 upon proteasome inhibition in cultured neurons.PLoS ONE 6,e22850(2011).
33.Di Giorgio,F.P.,Boulting,G.L.,Bobrowicz,S.& Eggan,K.C.Human Embryonic Stem Cell-Derived Motor Neurons Are Sensitive to the Toxic Effect of Glial Cells Carrying an ALS-Causing Mutation.Stem Cell 3,637-648(2008).
34.Amoroso,M.W.et al.Accelerated high-yield generation of limb-innervating motor neurons from human stem cells.J Neurosci 33,574-586(2013).
35.Chambers,S.M.et al.Highly efficient neural conversion of human ES and iPS cells by dual inhibition of SMAD signaling.Nat Biotechnol 27,275-280(2009).
36.Chambers,S.M.et al.Combined small-molecule inhibition accelerates developmental timing and converts human pluripotent stem cells into nociceptors.Nat Biotechnol 30,715-720(2012).
37.Mackenzie,I.R.A.et al.Pathological TDP-43 distinguishes sporadic amyotrophic lateral sclerosis from amyotrophic lateral sclerosis with SOD1 mutations.Ann Neurol.61,427-434(2007).
38.Love,M.I.,Huber,W.& Anders,S.Moderated estimation of fold change and dispersion for RNA-seq data with DESeq2.Genome Biology 15,550(2014).
39.Arnold,E.S.et al.ALS-linked TDP-43 mutations produce aberrant RNA splicing and adult-onset motor neuron disease without aggregation or loss of nuclear TDP-43.Proc.Natl.Acad.Sci.U.S.A.110,E736-45(2013).
40.Fiesel,F.C.,Weber,S.S.,Supper,J.,Zell,A.& Kahle,P.J.TDP-43 regulates global translational yield by splicing of exon junction complex component SKAR.Nucleic Acids Res 40,2668-2682(2012).
41.Prudencio,M.et al.Misregulation of human sortilin splicing leads to the generation of a nonfunctional progranulin receptor.P Natl Acad Sci Usa 109,21510-21515(2012).
42.Yang,C.et al.Partial loss of TDP-43 function causes phenotypes of amyotrophic lateral sclerosis.Proc.Natl.Acad.Sci.U.S.A.111,E1121-9(2014).
43.Bernard,E.,Jacob,L.,Mairal,J.& Vert,J.-P.Efficient RNA isoform identification and quantification from RNA-Seq data with network flows.Bioinformatics 30,2447-2455(2014).
44.Bryant,D.W.,Priest,H.D.& Mockler,T.C.Detection and quantification of alternative splicing variants using RNA-seq.Methods Mol Biol 883,97-110(2012).
45.Trapnell,C.et al.Differential analysis of gene regulation at transcript resolution with RNA-seq.Nat Biotechnol 31,46-53(2013).
46.Shiga,A.et al.Alteration of POLDIP3 Splicing Associated with Loss of Function of TDP-43 in Tissues Affected with ALS.PLoS ONE 7,(2012).
47.Grenningloh,G.,Soehrman,S.,Bondallaz,P.,Ruchti,E.& Cadas,H.Role of the microtubule destabilizing proteins SCG10 and stathmin in neuronal growth.J.Neurobiol.58,60-69(2004).
48.Shin,J.E.,Geisler,S.& DiAntonio,A.Dynamic regulation of SCG10 in regenerating axons after injury.Exp Neurol 252,1-11(2014).
49.Kasashima,K.,Sakashita,E.,Saito,K.& Sakamoto,H.Complex formation of the neuron-specific ELAV-like hu RNA-binding proteins.Nucleic Acids Res 30,4519-4526(2002).
50.Martin,K.R.et al.Over-expression of RCAN1 causes Down syndrome-like hippocampal deficits that alter learning and memory.Human Molecular Genetics 21,3025-3041(2012).
51.Ariyannur,P.S.et al.Methamphetamine-induced neuronal protein NAT8L is the NAA biosynthetic enzyme:implications for specialized acetyl coenzyme A metabolism in the CNS.Brain Research 1335,1-13(2010).
52.Boulting,G.L.et al.A functionally characterized test set of human induced pluripotent stem cells.Nat Biotechnol 29,279-286(2011).
53.Yuan,S.H.et al.Cell-surface marker signatures for the isolation of neural stem cells,glia and neurons derived from human pluripotent stem cells.PLoS ONE 6,e17540(2011).
54.Egawa,N.et al.Drug Screening for ALS Using Patient-Specific Induced Pluripotent Stem Cells.Sci Transl Med 4,145ra104-145ra104(2012).
55.Serio,A.et al.Astrocyte pathology and the absence of non-cell autonomy in an induced pluripotent stem cell model of TDP-43 proteinopathy.Proc.Natl.Acad.Sci.U.S.A.110,4697-4702(2013).
56.Bilican,B.et al.Mutant induced pluripotent stem cell lines recapitulate aspects of TDP-43 proteinopathies and reveal cell-specific vulnerability.Proc.Natl.Acad.Sci.U.S.A.109,5803-5808(2012).
57.Zhang,Z.et al.Downregulation of MicroRNA-9 in iPSC-Derived Neurons of FTD/ALS Patients with TDP-43 Mutations.PLoS ONE 8,e76055(2013).
58.Mason,M.,Lieberman,A.R.,Grenningloh,G.& Anderson,P.N.Transcriptional upregulation of SCG10 and CAP-23 is correlated with regeneration of the axons of peripheral and central neurons in vivo.Mol Cell Neurosci 20,595-615(2002).
59.Morii,H.,Shiraishi-Yamaguchi,Y.& Mori,N.SCG10,a microtubule destabilizing factor,stimulates the neurite outgrowth by modulating microtubule dynamics in rat hippocampal primary cultured neurons.J.Neurobiol.66,1101-1114(2006).
60.Shin,J.E.et al.SCG10 is a JNK target in the axonal degeneration pathway.P Natl Acad Sci Usa 109,E3696-E3705(2012).
61.Sobczak,A.et al.Calmyrin1 binds to SCG10 protein(stathmin2)to modulate neurite outgrowth.Biochim Biophys Acta 1813,1025-1037(2011).
62.Stein,R.,Mori,N.,Matthews,K.,Lo,L.C.& Anderson,D.J.The NGF-inducible SCG10 mRNA encodes a novel membrane-bound protein present in growth cones and abundant in developing neurons.Neuron 1,463-476(1988).
63.Bieche,I.et al.Expression of stathmin family genes in human tissues:non-neural-restricted expression for SCLIP.Genomics 81,400-410(2003).
64.Smith,B.N.et al.Exome-wide rare variant analysis identifies TUBA4A mutations associated with familial ALS.Neuron 84,324-331(2014).
65.Wu,C.-H.et al.Mutations in the profilin 1 gene cause familial amyotrophic lateral sclerosis.Nature 488,499-503(2012).
66.Nicolas,A.et al.Genome-wide Analyses Identify KIF5A as a Novel ALS Gene.Neuron 97,1268-1283.e6(2018).
67.Guerreiro,R.,Bras,J.& Hardy,J.SnapShot:Genetics of ALS and FTD.Cell 160,798-U485(2015).
68.Lagier-Tourenne,C.et al.Divergent roles of ALS-linked proteins FUS/TLS and TDP-43 intersect in processing long pre-mRNAs.Nat Neurosci 15,1488-1497(2012).
69.Lattante,S.,Rouleau,G.A.& Kabashi,E.TARDBP and FUS Mutations Associated with Amyotrophic Lateral Sclerosis:Summary and Update.Hum.Mutat.34,812-826(2013).
70.DeJesus-Hernandez,M.et al.Expanded GGGGCC hexanucleotide repeat in noncoding region of C9ORF72 causes chromosome 9p-linked FTD and ALS.Neuron 72,245-256(2011).
71.Renton,A.E.,Chio,A.& Traynor,B.J.State of play in amyotrophic lateral sclerosis genetics.Nat Neurosci 17,17-23(2014).
72.Renton,A.E.et al.A Hexanucleotide Repeat Expansion in C9ORF72 Is the Cause of Chromosome 9p21-Linked ALS-FTD.Neuron 72,257-268(2011).
73.Buratti,E.& Baralle,F.E.Multiple roles of TDP-43 in gene expression,splicing regulation,and human disease.Front Biosci 13,867-878(2008).
74.Sugiura,Y.& Mori,N.SCG10 expresses growth-associated manner in developing rat brain,but shows a different pattern to p19/stathmin or GAP-43.Brain Res.Dev.Brain Res.90,73-91(1995).
75.Levy,A.D.et al.Subcellular Golgi localization of stathmin family proteins is promoted by a specific set of DHHC palmitoyl transferases.Mol Biol Cell 22,1930-1942(2011).
76.Taylor,J.P.,Brown,R.H.& Cleveland,D.W.Decoding ALS:from genes to mechanism.Nature 539,197-206(2016).
77.Chauvin,S.& Sobel,A.Neuronal stathmins:A family of phosphoproteins cooperating for neuronal development,plasticity and regeneration.Progress in Neurobiology 126,1-18(2015).
78.Meijering,E.et al.Design and validation of a tool for neurite tracing and analysis in fluorescence microscopy images.Cytometry Part A 58A,167-176(2004).
79.Taylor,A.M.et al.A microfluidic culture platform for CNS axonal injury,regeneration and transport.Nat Methods 2,599-605(2005).
80.Ling,J.P.,Pletnikova,O.,Troncoso,J.C.& Wong,P.C.TDP-43 repression of nonconserved cryptic exons is compromised in ALS-FTD.Science 349,650-655(2015).
81.Humphrey,J.,Emmett,W.,Fratta,P.,Isaacs,A.M.& Plagnol,V.Quantitative analysis of cryptic splicing associated with TDP-43 depletion.BMC Med Genomics 10,38(2017).
82.Rabin,S.J.et al.Sporadic ALS has compartment-specific aberrant exon splicing and altered cell-matrix adhesion biology.Human Molecular Genetics 19,313-328(2009).
83.Highley,J.R.et al.Loss of nuclear TDP-43 in amyotrophic lateral sclerosis(ALS)causes altered expression of splicing machinery and widespread dysregulation of RNA splicing in motor neurones.Neuropathology and Applied Neurobiology 40,670-685(2014).
84.D’Erchia,A.M.et al.Massive transcriptome sequencing of human spinal cord tissues provides new insights into motor neuron degeneration in ALS.Sci Rep 7,10046(2017).
85.Henriques,A.,Pitzer,C.& Schneider,A.Neurotrophic growth factors for the treatment of amyotrophic lateral sclerosis:where do we stand? Front Neurosci 4,32(2010).
86.Kaplan,A.et al.Neuronal Matrix Metalloproteinase-9 Is a Determinant of Selective Neurodegeneration.Neuron 81,333-348(2014).
87.Markmiller,S.et al.Context-Dependent and Disease-Specific Diversity in Protein Interactions within Stress Granules.Cell 172,590-604.e13(2018).
88.Taylor,J.P.,Brown,R.H.& Cleveland,D.W.Decoding ALS:from genes to mechanism.Nature 539,197-206(2016).
89.de Boer,A.S.et al.Genetic validation of a therapeutic target in a mouse model of ALS.Sci Transl Med 6,248ra104-248ra104(2014).
90.Steinbaugh,M.J.et al.bcbioRNASeq:R package for bcbio RNA-seq analysis.F1000Research 6,1976(2017).
91.Patro,R.,Duggal,G.,Love,M.I.,Irizarry,R.A.& Kingsford,C.Salmon provides fast and bias-aware quantification of transcript expression.Nat Methods 14,417-419(2017).
92.Soneson,C.,Love,M.I.& Robinson,M.D.Differential analyses for RNA-seq:transcript-level estimates improve gene-level inferences.F1000Research 4,1521(2016).
93.Benjamini,Y.& Hochberg,Y.Controlling the False Discovery Rate:A Practical and Powerful Approach to Multiple Testing.http://www.jstor.org/stable/2346101 1,289-300(1995).
94.Son,E.Y.et al.Conversion of mouse and human fibroblasts into functional spinal motor neurons.Cell Stem Cell 9,205-218(2011).
95.Labun,K.,Montague,T.G.,Gagnon,J.A.,Thyme,S.B.& Valen,E.CHOPCHOP v2:a web tool for the next generation of CRISPR genome engineering.Nucleic Acids Res 44,W272-W276(2016).
96.Ferreira,T.A.et al.Neuronal morphometry directly from bitmap images.Nat Methods 11,982-984(2014).
1.Pasinelli,P.& Brown,R.H.Molecular biology of amyotrophic lateral sclerosis:insights from genetics.Nat.Rev.Neurosci.7,710-723(2006).
2.Rowland,L.P.& Shneider,N.A.Amyotrophic lateral sclerosis.New England Journal of Medicine 344,1688-1700(2001).
3.Ravits,J.et al.Deciphering amyotrophic lateral sclerosis:What phenotype,neuropathology and genetics are telling us about pathogenesis.Amyotroph Lateral Scler Frontotemporal Degener 14,5-18(2013).
4.Miller,R.G.,Mitchell,J.D.& Moore,D.H.Riluzole for amyotrophic lateral sclerosis(ALS)/motor neuron disease(MND).Cochrane Database Syst Rev 3,CD001447(2012).
5.Ling,S.-C.,Polymenidou,M.& Cleveland,D.W.Converging mechanisms in ALS and FTD:disrupted RNA and protein homeostasis.Neuron 79,416-438(2013).
6.Dion,P.A.,Daoud,H.& Rouleau,G.A.Genetics of motor neuron disorders:new insights into pathogenic mechanisms.Nat.Rev.Genet.10,769-782(2009).
7.Neumann,M.et al.Ubiquitinated TDP-43 in frontotemporal lobar degeneration and amyotrophic lateral sclerosis.Science 314,130-133(2006).
8.Chen-Plotkin,A.S.,Lee,V.M.-Y.& Trojanowski,J.Q.TAR DNA-binding protein 43 in neurodegenerative disease.Nature Reviews Neurology 6,211-220(2010).
9.Ignatius,S.H.,Wu,F.,Harrich,D.,GarciaMartinez,L.F.& Gaynor,R.B.Cloning and Characterization of a Novel Cellular Protein,Tdp-43,That Binds to Human-Immunodeficiency-Virus Type-1 Tar Dna-Sequence Motifs.J Virol 69,3584-3596(1995).
10.Buratti,E.et al.Nuclear factor TDP-43 and SR proteins promote in vitro and in vivo CFTR exon 9 skipping.EMBO J 20,1774-1784(2001).
11.Polymenidou,M.et al.Long pre-mRNA depletion and RNA missplicing contribute to neuronal vulnerability from loss of TDP-43.Nat Neurosci 14,459-468(2011).
12.Kawahara,Y.& Mieda-Sato,A.TDP-43 promotes microRNA biogenesis as a component of the Drosha and Dicer complexes.P Natl Acad Sci Usa 109,3347-3352(2012).
13.Liu-Yesucevitz,L.et al.Tar DNA Binding Protein-43(TDP-43)Associates with Stress Granules:Analysis of Cultured Cells and Pathological Brain Tissue.PLoS ONE 5,(2010).
14.Parker,S.J.et al.Endogenous TDP-43 localized to stress granules can subsequently form protein aggregates.Neurochem.Int.60,415-424(2012).
15.Alami,N.H.et al.Axonal transport of TDP-43 mRNA granules is impaired by ALS-causing mutations.Neuron 81,536-543(2014).
16.Volkening,K.,Leystra-Lantz,C.,Yang,W.,Jaffee,H.& Strong,M.J.Tar DNA binding protein of 43 kDa(TDP-43),14-3-3 proteins and copper/zinc superoxide dismutase(SOD1)interact to modulate NFL mRNA stability.Implications for altered RNA processing in amyotrophic lateral sclerosis(ALS).Brain Research 1305,168-182(2009).
17.Benajiba,L.et al.TARDBP mutations in motoneuron disease with frontotemporal lobar degeneration.Ann Neurol.65,470-473(2009).
18.Rutherford,N.J.et al.Novel Mutations in TARDBP(TDP-43)in Patients with Familial Amyotrophic Lateral Sclerosis.PLoS Genet 4,(2008).
19.Sreedharan,J.et al.TDP-43 mutations in familial and sporadic amyotrophic lateral sclerosis.Science 319,1668-1672(2008).
20.Van Deerlin,V.M.et al.TARDBP mutations in amyotrophic lateral sclerosis with TDP-43 neuropathology:a genetic and histopathological analysis.The Lancet Neurology 7,409-416(2008).
21.Yokoseki,A.et al.TDP-43 mutation in familial amyotrophic lateral sclerosis.Ann Neurol.63,538-542(2008).
22.Lee,E.B.,Lee,V.M.-Y.& Trojanowski,J.Q.Gains or losses:molecular mechanisms of TDP43-mediated neurodegeneration.Nat.Rev.Neurosci.13,38-50(2012).
23.Kraemer,B.C.et al.Loss of murine TDP-43 disrupts motor function and plays an essential role in embryogenesis.Acta Neuropathol 119,409-419(2010).
24.Sephton,C.F.et al.TDP-43 is a developmentally regulated protein essential for early embryonic development.J.Biol.Chem.285,6826-6834(2010).
25.Wu, L.-S., Cheng, W.-C.& Shen, C.-K.J.Targeted depletion of TDP-43 expression in the spinal cord motor neurons leads to the development of amyotrophic lateral sclerosis-like phenotypes in mice.J.Biol.Chem.287,27335-27344(2012).
26.Yang,C.et al.Partial loss of TDP-43 function causes phenotypes of amyotrophic lateral sclerosis.Proc.Natl.Acad.Sci.U.S.A.111,E1121-9(2014).
27.Iguchi,Y.et al.Loss of TDP-43 causes age-dependent progressive motor neuron degeneration.Brain 136,1371-1382(2013).
28.Tollervey,J.R.et al.Characterizing the RNA targets and position-dependent splicing regulation by TDP-43.Nat Neurosci 14,452-458(2011).
29.Davis-Dusenbery,B.N.,Williams,L.A.,Klim,J.R.& Eggan,K.How to make spinal motor neurons.Development 141,491-501(2014).
30.Han, S.S.W., Williams, L.A.& Eggan, K.C.Constructing and deconstructing stem cell models of neurological disease.Neuron 70,626-644(2011).
31.Kiskinis,E.et al.Pathways disrupted in human ALS motor neurons identified through genetic correction of mutant SOD1.Cell Stem Cell 14,781-795(2014).
32.van Eersel,J.et al.Cytoplasmic accumulation and aggregation of TDP-43 upon proteasome inhibition in cultured neurons.PLoS ONE 6,e22850(2011).
33.Di Giorgio,F.P.,Boulting,G.L.,Bobrowicz,S.& Eggan,K.C.Human Embryonic Stem Cell-Derived Motor Neurons Are Sensitive to the Toxic Effect of Glial Cells Carrying an ALS-Causing Mutation.Stem Cell 3,637-648(2008).
34.Amoroso,M.W.et al.Accelerated high-yield generation of limb-innervating motor neurons from human stem cells.J Neurosci 33,574-586(2013).
35.Chambers,S.M.et al.Highly efficient neural conversion of human ES and iPS cells by dual inhibition of SMAD signaling.Nat Biotechnol 27,275-280(2009).
36.Chambers,S.M.et al.Combined small-molecule inhibition accelerates developmental timing and converts human pluripotent stem cells into nociceptors.Nat Biotechnol 30,715-720(2012).
37.Mackenzie,I.R.A.et al.Pathological TDP-43 distinguishes sporadic amyotrophic lateral sclerosis from amyotrophic lateral sclerosis with SOD1 mutations.Ann Neurol.61,427-434(2007).
38.Love,M.I.,Huber,W.& Anders,S.Moderated estimation of fold change and dispersion for RNA-seq data with DESeq2.Genome Biology 15,550(2014).
39.Arnold,E.S.et al.ALS-linked TDP-43 mutations produce aberrant RNA splicing and adult-onset motor neuron disease without aggregation or loss of nuclear TDP-43.Proc.Natl.Acad.Sci.U.S.A.110,E736-45(2013).
40.Fiesel,F.C.,Weber,S.S.,Supper,J.,Zell,A.& Kahle,P.J.TDP-43 regulates global translational yield by splicing of exon junction complex component SKAR.Nucleic Acids Res 40,2668-2682(2012).
41.Prudencio,M.et al.Misregulation of human sortilin splicing leads to the generation of a nonfunctional progranulin receptor.P Natl Acad Sci Usa 109,21510-21515(2012).
42.Yang,C.et al.Partial loss of TDP-43 function causes phenotypes of amyotrophic lateral sclerosis.Proc.Natl.Acad.Sci.U.S.A.111,E1121-9(2014).
43.Bernard,E.,Jacob,L.,Mairal,J.& Vert,J.-P.Efficient RNA isoform identification and quantification from RNA-Seq data with network flows.Bioinformatics 30,2447-2455(2014).
44.Bryant,D.W.,Priest,H.D.& Mockler,T.C.Detection and quantification of alternative splicing variants using RNA-seq.Methods Mol Biol 883,97-110(2012).
45.Trapnell,C.et al.Differential analysis of gene regulation at transcript resolution with RNA-seq.Nat Biotechnol 31,46-53(2013).
46.Shiga,A.et al.Alteration of POLDIP3 Splicing Associated with Loss of Function of TDP-43 in Tissues Affected with ALS.PLoS ONE 7,(2012).
47.Grenningloh,G.,Soehrman,S.,Bondallaz,P.,Ruchti,E.& Cadas,H.Role of the microtubule destabilizing proteins SCG10 and stathmin in neuronal growth.J.Neurobiol.58,60-69(2004).
48.Shin,J.E.,Geisler,S.& DiAntonio,A.Dynamic regulation of SCG10 in regenerating axons after injury.Exp Neurol 252,1-11(2014).
49.Kasashima,K.,Sakashita,E.,Saito,K.& Sakamoto,H.Complex formation of the neuron-specific ELAV-like hu RNA-binding proteins.Nucleic Acids Res 30,4519-4526(2002).
50.Martin,K.R.et al.Over-expression of RCAN1 causes Down syndrome-like hippocampal deficits that alter learning and memory.Human Molecular Genetics 21,3025-3041(2012).
51.Ariyannur,P.S.et al.Methamphetamine-induced neuronal protein NAT8L is the NAA biosynthetic enzyme:implications for specialized acetyl coenzyme A metabolism in the CNS.Brain Research 1335,1-13(2010).
52.Boulting,G.L.et al.A functionally characterized test set of human induced pluripotent stem cells.Nat Biotechnol 29,279-286(2011).
53.Yuan,S.H.et al.Cell-surface marker signatures for the isolation of neural stem cells,glia and neurons derived from human pluripotent stem cells.PLoS ONE 6,e17540(2011).
54.Egawa,N.et al.Drug Screening for ALS Using Patient-Specific Induced Pluripotent Stem Cells.Sci Transl Med 4,145ra104-145ra104(2012).
55.Serio,A.et al.Astrocyte pathology and the absence of non-cell autonomy in an induced pluripotent stem cell model of TDP-43 proteinopathy.Proc.Natl.Acad.Sci.U.S.A.110,4697-4702(2013).
56.Bilican,B.et al.Mutant induced pluripotent stem cell lines recapitulate aspects of TDP-43 proteinopathies and reveal cell-specific vulnerability.Proc.Natl.Acad.Sci.U.S.A.109,5803-5808(2012).
57.Zhang,Z.et al.Downregulation of MicroRNA-9 in iPSC-Derived Neurons of FTD/ALS Patients with TDP-43 Mutations.PLoS ONE 8,e76055(2013).
58.Mason,M.,Lieberman,A.R.,Grenningloh,G.& Anderson,P.N.Transcriptional upregulation of SCG10 and CAP-23 is correlated with regeneration of the axons of peripheral and central neurons in vivo.Mol Cell Neurosci 20,595-615(2002).
59.Morii,H.,Shiraishi-Yamaguchi,Y.& Mori,N.SCG10,a microtubule destabilizing factor,stimulates the neurite outgrowth by modulating microtubule dynamics in rat hippocampal primary cultured neurons.J.Neurobiol.66,1101-1114(2006).
60.Shin,J.E.et al.SCG10 is a JNK target in the axonal degeneration pathway.P Natl Acad Sci Usa 109,E3696-E3705(2012).
61.Sobczak,A.et al.Calmyrin1 binds to SCG10 protein(stathmin2)to modulate neurite outgrowth.Biochim Biophys Acta 1813,1025-1037(2011).
62.Stein,R.,Mori,N.,Matthews,K.,Lo,L.C.& Anderson,D.J.The NGF-inducible SCG10 mRNA encodes a novel membrane-bound protein present in growth cones and abundant in developing neurons.Neuron 1,463-476(1988).
63.Bieche,I.et al.Expression of stathmin family genes in human tissues:non-neural-restricted expression for SCLIP.Genomics 81,400-410(2003).
64.Smith,B.N.et al.Exome-wide rare variant analysis identifies TUBA4A mutations associated with familial ALS.Neuron 84,324-331(2014).
65.Wu,C.-H.et al.Mutations in the profilin 1 gene cause familial amyotrophic lateral sclerosis.Nature 488,499-503(2012).
66.Nicolas,A.et al.Genome-wide Analyses Identify KIF5A as a Novel ALS Gene.Neuron 97,1268-1283.e6(2018).
67.Guerreiro,R.,Bras,J.& Hardy,J.SnapShot:Genetics of ALS and FTD.Cell 160,798-U485(2015).
68.Lagier-Tourenne,C.et al.Divergent roles of ALS-linked proteins FUS/TLS and TDP-43 intersect in processing long pre-mRNAs.Nat Neurosci 15,1488-1497(2012).
69.Lattante,S.,Rouleau,G.A.& Kabashi,E.TARDBP and FUS Mutations Associated with Amyotrophic Lateral Sclerosis:Summary and Update.Hum.Mutat.34,812-826(2013).
70.DeJesus-Hernandez,M.et al.Expanded GGGGCC hexanucleotide repeat in noncoding region of C9ORF72 causes chromosome 9p-linked FTD and ALS.Neuron 72,245-256(2011).
71.Renton,A.E.,Chio,A.& Traynor,B.J.State of play in amyotrophic lateral sclerosis genetics.Nat Neurosci 17,17-23(2014).
72.Renton,A.E.et al.A Hexanucleotide Repeat Expansion in C9ORF72 Is the Cause of Chromosome 9p21-Linked ALS-FTD.Neuron 72,257-268(2011).
73.Buratti,E.& Baralle,F.E.Multiple roles of TDP-43 in gene expression,splicing regulation,and human disease.Front Biosci 13,867-878(2008).
74.Sugiura,Y.& Mori,N.SCG10 expresses growth-associated manner in developing rat brain,but shows a different pattern to p19/stathmin or GAP-43.Brain Res.Dev.Brain Res.90,73-91(1995).
75.Levy,A.D.et al.Subcellular Golgi localization of stathmin family proteins is promoted by a specific set of DHHC palmitoyl transferases.Mol Biol Cell 22,1930-1942(2011).
76.Taylor,J.P.,Brown,R.H.& Cleveland,D.W.Decoding ALS:from genes to mechanism.Nature 539,197-206(2016).
77.Chauvin,S.& Sobel,A.Neuronal stathmins:A family of phosphoproteins cooperating for neuronal development,plasticity and regeneration.Progress in Neurobiology 126,1-18(2015).
78.Meijering,E.et al.Design and validation of a tool for neurite tracing and analysis in fluorescence microscopy images.Cytometry Part A 58A,167-176(2004).
79.Taylor,A.M.et al.A microfluidic culture platform for CNS axonal injury,regeneration and transport.Nat Methods 2,599-605(2005).
80.Ling,J.P.,Pletnikova,O.,Troncoso,J.C.& Wong,P.C.TDP-43 repression of nonconserved cryptic exons is compromised in ALS-FTD.Science 349,650-655(2015).
81.Humphrey,J.,Emmett,W.,Fratta,P.,Isaacs,A.M.& Plagnol,V.Quantitative analysis of cryptic splicing associated with TDP-43 depletion.BMC Med Genomics 10,38(2017).
82.Rabin,S.J.et al.Sporadic ALS has compartment-specific aberrant exon splicing and altered cell-matrix adhesion biology.Human Molecular Genetics 19,313-328(2009).
83.Highley,J.R.et al.Loss of nuclear TDP-43 in amyotrophic lateral sclerosis(ALS)causes altered expression of splicing machinery and widespread dysregulation of RNA splicing in motor neurones.Neuropathology and Applied Neurobiology 40,670-685(2014).
84.D’Erchia,A.M.et al.Massive transcriptome sequencing of human spinal cord tissues provides new insights into motor neuron degeneration in ALS.Sci Rep 7,10046(2017).
85.Henriques,A.,Pitzer,C.& Schneider,A.Neurotrophic growth factors for the treatment of amyotrophic lateral sclerosis:where do we stand? Front Neurosci 4,32(2010).
86.Kaplan,A.et al.Neuronal Matrix Metalloproteinase-9 Is a Determinant of Selective Neurodegeneration.Neuron 81,333-348(2014).
87.Markmiller,S.et al.Context-Dependent and Disease-Specific Diversity in Protein Interactions within Stress Granules.Cell 172,590-604.e13(2018).
88.Taylor,J.P.,Brown,R.H.& Cleveland,D.W.Decoding ALS:from genes to mechanism.Nature 539,197-206(2016).
89.de Boer,A.S.et al.Genetic validation of a therapeutic target in a mouse model of ALS.Sci Transl Med 6,248ra104-248ra104(2014).
90.Steinbaugh,M.J.et al.bcbioRNASeq:R package for bcbio RNA-seq analysis.F1000Research 6,1976(2017).
91.Patro,R.,Duggal,G.,Love,M.I.,Irizarry,R.A.& Kingsford,C.Salmon provides fast and bias-aware quantification of transcript expression.Nat Methods 14,417-419(2017).
92.Soneson,C.,Love,M.I.& Robinson,M.D.Differential analyses for RNA-seq:transcript-level estimates improve gene-level inferences.F1000Research 4,1521(2016).
93.Benjamini,Y.& Hochberg,Y.Controlling the False Discovery Rate:A Practical and Powerful Approach to Multiple Testing.http://www.jstor.org/stable/2346101 1,289-300(1995).
94.Son,E.Y.et al.Conversion of mouse and human fibroblasts into functional spinal motor neurons.Cell Stem Cell 9,205-218(2011).
95.Labun,K.,Montague,T.G.,Gagnon,J.A.,Thyme,S.B.& Valen,E.CHOPCHOP v2:a web tool for the next generation of CRISPR genome engineering.Nucleic Acids Res 44,W272-W276(2016).
96.Ferreira,T.A.et al.Neuronal morphometry directly from bitmap images.Nat Methods 11,982-984(2014).
実施例2:
近年、ヒト運動ニューロンにおけるRNA結合タンパク質TDP-43によって調節されたmRNA転写物の同定が報告された。Klim,J.R.,et al.を参照されたい。ALS関連タンパク質TDP-43は、運動ニューロンの成長及び修復のメディエーターであるSTMN2のレベルを維持する。Nat Neurosci,2019.22(2):p.167-179。TDP-43はヒト運動ニューロン中の数百の転写物を調節するが、TDP-43枯渇により最も影響を受けた転写物のうちの1つはSTMN2であった。STMN2は微小管会合に関与するタンパク質であり、ニューロンによって発現される最も豊富な転写物のうちの1つである。データの詳細な分析により、TDP-43がSTMN2転写物中の潜在性エクソンを抑制することが明らかとなった。この潜在性エクソンの包含により、完全長形態の発現が防止され、STMN2タンパク質のレベルの劇的な低下がもたらされる。細胞培養物におけるTDP-43のノックダウン、及びTDP-43病変を示す患者由来の死後組織は、STMN2スプライシングの変化を示す。潜在性エクソン含有転写物は、それ自体の終止部位及び開始部位を含有しているため、17アミノ酸ペプチドをコードしている可能性がある。ヒトモデルにおけるこの変化を、死後脊髄由来のRNAシーケンシングデータで検証した。このため、潜在性STMN2転写物またはそれがコードするペプチドが、ALSを発症しているかもしくはALSを有する人々、またはTDP-43タンパク質症(例えば、パーキンソン病、外傷性脳損傷、アルツハイマー病)を示す他の患者のCSF/体液バイオマーカーとして機能し得るか否かを考察した。
近年、ヒト運動ニューロンにおけるRNA結合タンパク質TDP-43によって調節されたmRNA転写物の同定が報告された。Klim,J.R.,et al.を参照されたい。ALS関連タンパク質TDP-43は、運動ニューロンの成長及び修復のメディエーターであるSTMN2のレベルを維持する。Nat Neurosci,2019.22(2):p.167-179。TDP-43はヒト運動ニューロン中の数百の転写物を調節するが、TDP-43枯渇により最も影響を受けた転写物のうちの1つはSTMN2であった。STMN2は微小管会合に関与するタンパク質であり、ニューロンによって発現される最も豊富な転写物のうちの1つである。データの詳細な分析により、TDP-43がSTMN2転写物中の潜在性エクソンを抑制することが明らかとなった。この潜在性エクソンの包含により、完全長形態の発現が防止され、STMN2タンパク質のレベルの劇的な低下がもたらされる。細胞培養物におけるTDP-43のノックダウン、及びTDP-43病変を示す患者由来の死後組織は、STMN2スプライシングの変化を示す。潜在性エクソン含有転写物は、それ自体の終止部位及び開始部位を含有しているため、17アミノ酸ペプチドをコードしている可能性がある。ヒトモデルにおけるこの変化を、死後脊髄由来のRNAシーケンシングデータで検証した。このため、潜在性STMN2転写物またはそれがコードするペプチドが、ALSを発症しているかもしくはALSを有する人々、またはTDP-43タンパク質症(例えば、パーキンソン病、外傷性脳損傷、アルツハイマー病)を示す他の患者のCSF/体液バイオマーカーとして機能し得るか否かを考察した。
図17A~17Cは、RNAをCSF由来エクソソームから容易に採取し、次いで、cDNAに変換し、完全STMN2転写物及び潜在性STMN2転写物ならびに正規化のための対照RNAについてアッセイすることができることを示す(図17A)。TaqMan Q-RT-PCRアッセイを、このアッセイがヒトニューロン中でTDP-43ノックダウンアプローチを使用して完全STMN2転写物及び潜在性STMN2転写物の両方を同時に検出することを示すために検証した。STMN2転写物をハウスキーピングリボソームサブユニットRNA18S5に対して正規化する。TDP-43の細胞を枯渇させるアンチセンスオリゴヌクレオチド(ASO)またはTDP-43ノックダウンを誘導するsiRNAのいずれかを使用して、培養ヒトニューロン中のTDP-43レベルを低減させた。両方の条件において、対照と比較した潜在性エクソンの強力な誘導が確認された(図17B)。検証済みのマルチプレックスqPCRアッセイを使用して、次に、300ulの患者試料を使用してCSF由来エクソソームからRNAを単離し、潜在性STMN2のレベルを判定した(n=健常対照7例、n=疾患擬態2例、及びn=ALS患者9例)。対照試料と比較して、大部分のALS試料はSTMN2潜在性エクソンの平均レベルを上回っていることを示し、いくつかの試料は数桁高いレベルを示した(図17C)。この比較的少ない試料のセットにおいてでさえ、ALS患者における潜在性エクソン発現の増加が極めて有意であった(P<0.005)ことに留意されたい。非ALS運動ニューロン疾患(擬態)を有する個体2例が対照レベルのスプライシングを示したことは更に注目に値する。最後に、患者データには興味深い「性質(texture)」があり、高レベルの発現を示す患者もいれば、より正常なレベルを示す患者もいる。比較的低レベルの患者は、その疾患の初期であるか、または非TDP-43疾患を有しているかのいずれかであり得るという仮説が立てられている。
ALSの最も一般的な病理学的特徴は、TDP-43の細胞質蓄積及び核クリアランスである。多くのグループ及び企業は、TDP-43の局在化及び機能におけるこれらの変化をレスキューする治療薬の開発に関心がある。しかしながら、これまでのところ、TDP-43機能障害またはそのレスキューをモニタリングするために生存している人に使用することができるバイオマーカーは存在しない。ここで説明するアッセイは、まさにこの方法で使用することができる。更に、ALSにおける標的としてのSTMN2及びその潜在性スプライシング自体に関心が向けられている。このアッセイによって、臨床試験中の患者において標的の関与を直接測定することが可能になる。
実施例3
患者の背景
患者は現在40歳の男性であり、ALSの症状は、左手の脱力感を伴って2017年4月に最初に始まった。脱力感は次第に悪化し、両手及び両腕の萎縮を伴うまでに広がった。2018年5月頃、患者は脚の痙縮、脱力感、及び萎縮、ならびに構音障害を発症し、これらは次第に悪化した。ALSの診断が2017年11月に臨床的に確定し、2018年3月にEMG検査によって確認された。ALSの家族歴はなく、包括的なエクソーム及びゲノムスキャンでは、C9ORF72またはSOD1遺伝子の変異などの、ALSの原因となると証明されている変異は明らかにならなかった。
患者の背景
患者は現在40歳の男性であり、ALSの症状は、左手の脱力感を伴って2017年4月に最初に始まった。脱力感は次第に悪化し、両手及び両腕の萎縮を伴うまでに広がった。2018年5月頃、患者は脚の痙縮、脱力感、及び萎縮、ならびに構音障害を発症し、これらは次第に悪化した。ALSの診断が2017年11月に臨床的に確定し、2018年3月にEMG検査によって確認された。ALSの家族歴はなく、包括的なエクソーム及びゲノムスキャンでは、C9ORF72またはSOD1遺伝子の変異などの、ALSの原因となると証明されている変異は明らかにならなかった。
患者は、FDAが承認した3つのALS治療薬であるリルゾール、エダラボン、及びニューデクスタを服用している。更に、患者は2019年6月及び11月に韓国で自家間葉系幹細胞による処置を受けた。前述の治療にもかかわらず、患者の臨床経過及びALSFRSの経過は加速している。
プロジェクトの論理的根拠
スタスミン2(STMN2)は、微小管の安定性を制御する、CNS(脊髄運動ニューロンで特に顕著)でのみ発現する179アミノ酸のタンパク質である。SCG10(上頸神経節10)として長年研究されているSTMN2は、損傷後の軸索再成長に不可欠である。驚くべきことに、スタスミン2の機能が、散発性ALSの多くの症例、ならびにTDP43及びC9ORF72をコードする遺伝子の変異に起因するALSにおいて抑制されることが、2019年に2つの重要な論文により別々に証明された(1、2)。これらの知見は、最近、第3のラボによって独立して確認された(3)。
スタスミン2(STMN2)は、微小管の安定性を制御する、CNS(脊髄運動ニューロンで特に顕著)でのみ発現する179アミノ酸のタンパク質である。SCG10(上頸神経節10)として長年研究されているSTMN2は、損傷後の軸索再成長に不可欠である。驚くべきことに、スタスミン2の機能が、散発性ALSの多くの症例、ならびにTDP43及びC9ORF72をコードする遺伝子の変異に起因するALSにおいて抑制されることが、2019年に2つの重要な論文により別々に証明された(1、2)。これらの知見は、最近、第3のラボによって独立して確認された(3)。
重要なことに、これらの研究により、ヒト運動ニューロンにおける最も豊富な転写物の1つであるSTMN2が、TDP-43と相互作用する中心的RNAとして同定された。これらはまた、老化、環境への曝露、損傷、またはALS/FTDの原因となる変異に起因するタンパク質恒常性の破壊が、TDP43の誤局在化、凝集、及びRNA代謝の変化(ほぼ全ての散発性ALS症例に存在する病態)を招くという、散発性ALSにおける機序にそれぞれ裏付けを与えた。TDP-43機能の喪失により多くの転写物の存在量が変化するが、TDP-43ノックダウンまたは機能喪失後のSTMN2の急激な喪失は、STMN2をTDP-43病変及び軸索を保護しニューロパチーを予防する機序の破壊に結び付ける説得力のあるエビデンスを提供する。
この印象的な最近の文献を踏まえて、患者から組織をサンプリングし、患者の運動ニューロンへの影響をモデル化するための培養条件を考案した。この経路及び患者の細胞を対象とした一連の試験を、エクソン1と2の間のイントロンでTDP-43がSTMN2 プレmRNAに結合するSTMN2のTDP-43調節の機序を試験するために行った。TDP-43レベルの低減または核外輸送のいずれかは、潜在性エクソンの早期のポリアデニル化及びスプライシングにより、完全長転写物を代償としてトランケートされたSTMN2 mRNA転写物がもたらされるという、STMN2に関する同じ結果を招く(図81)。したがって、脊髄性筋萎縮症に対するヌシネルセンの成功を考慮すると、STMN2のTDP-43調節は、疾患バイオマーカーとして、または更にはスプライススイッチングアンチセンスオリゴヌクレオチドの治療標的として機能する可能性があるように思われる。
大規模スクリーニング後、3つのASOのパネルを同定した。うち1つ(SJ+94)は、(i)患者の運動ニューロンにおけるTDP-43誘導性STMN2ミススプライシングを効果的に補正し、(ii)非毒性である。パネル内の他の2つのASOについても、更に分析を実施した。
患者の運動ニューロンは、健常個体と比較した場合に核内TDP-43が少ない
SJ+94及びSJ-1を含むパネル内のASOに最終的に至った科学的発見は、(1)散発性ALS患者はTDP-43が誤局在化していること、すなわち、健常個体と比較した場合に核内TDP-43が少ないこと、及び(2)このTDP-43の誤局在化が、散発性ALS患者において患者の疾患進行を促進するトランケートされた潜在性STMN2をもたらす、STMN2のミススプライシングの原因となることである。
SJ+94及びSJ-1を含むパネル内のASOに最終的に至った科学的発見は、(1)散発性ALS患者はTDP-43が誤局在化していること、すなわち、健常個体と比較した場合に核内TDP-43が少ないこと、及び(2)このTDP-43の誤局在化が、散発性ALS患者において患者の疾患進行を促進するトランケートされた潜在性STMN2をもたらす、STMN2のミススプライシングの原因となることである。
患者から提供された細胞から細胞をリプログラミングして、人工多能性幹細胞(iPSC)MGH 138を作製した(図84A)。幹細胞株(MGH 138)の遺伝子型が患者のものであることを、配列解析を使用して確認した(図84B)。この確認の上で、幹細胞由来の運動ニューロン(hMN)を患者のiPS細胞から作製した(図84C~84D)。次に、患者の運動ニューロンを、本明細書に記載のin vitro概念実証試験の全てに使用した。
患者の運動ニューロンを作製後、患者の運動ニューロンと健常対照の核内TDP-43に何らかの差異があるか否かを確認することを決定した。前述の通り、細胞質誤局在化として現れる可能性がある核内TDP-43の喪失は、死後CNS組織の複数の分析に基づく散発性ALSの病理学的特徴である。運動ニューロン中での検出は死後組織よりもはるかに困難であるが、少なくとも1つの先行研究では、ALS患者のiPSC由来ニューロンが、TDP-43病変(その細胞質誤局在化を含む)を再現できることが報告されている。
患者のiPS細胞及び健常対照5例のiPSC細胞株からニューロンを単離した。免疫細胞化学を使用して、ニューロンにおけるTDP-43の細胞内局在化を探索した(図85A)。対照ニューロンでは、ピアソン係数分析を用いて主に核内TDP-43染色が観察され、これによりTDP-43免疫染色とDNA対比染色との間の強い相関が明らかとなった(図85B)。対照的に、患者iPS細胞由来ニューロンは、TDP-43と核染色との間の相関の減少を示し、これは、対照と比較して患者の運動ニューロンにおける核内TDP-43のレベルが低いことを示すものであり、患者におけるTDP-43病変が確認された(図85B)。
患者特異的in vitroモデル
過去2年間にわたって、公開された3つの独立した試験により、散発性ALS患者における核内TDP-43の枯渇がSTMN2のトランケーションを引き起こすことが示された。しかしながら、これらの試験には、散発性ALS患者の死後組織が含まれていた。そのため、患者の運動ニューロンを試験して、患者のSTMN2がTDP-43によって同様に調節されているか否かを確認した。したがって、患者の運動ニューロンの核内TDP-43レベルが非ALS対照と比較して低減していることが実証されているが、患者の運動ニューロンにおける潜在性STMN2を抑制する際の(もしあれば、考えられるASOの)有効性をより明確に評価するために、このレベルをin vitro細胞アッセイにおいて更に低減させた。TDP-43及びSTMN2が機能不全であるという決定的な確証には、CNS組織の詳細な分析及び切開が必要であり、これは生存ALS患者に対しては選択されないことから、このアプローチが必要であった。更に、このin vitroアプローチは、散発性ALS患者におけるin vivo TDP-43病変(機能的TDP-43の喪失)と完全に一致している。
過去2年間にわたって、公開された3つの独立した試験により、散発性ALS患者における核内TDP-43の枯渇がSTMN2のトランケーションを引き起こすことが示された。しかしながら、これらの試験には、散発性ALS患者の死後組織が含まれていた。そのため、患者の運動ニューロンを試験して、患者のSTMN2がTDP-43によって同様に調節されているか否かを確認した。したがって、患者の運動ニューロンの核内TDP-43レベルが非ALS対照と比較して低減していることが実証されているが、患者の運動ニューロンにおける潜在性STMN2を抑制する際の(もしあれば、考えられるASOの)有効性をより明確に評価するために、このレベルをin vitro細胞アッセイにおいて更に低減させた。TDP-43及びSTMN2が機能不全であるという決定的な確証には、CNS組織の詳細な分析及び切開が必要であり、これは生存ALS患者に対しては選択されないことから、このアプローチが必要であった。更に、このin vitroアプローチは、散発性ALS患者におけるin vivo TDP-43病変(機能的TDP-43の喪失)と完全に一致している。
患者のSTMN2がTDP-43により調節されているか否かを試験するために、患者の運動ニューロンをsiTARDBP RNAで処置してTDP-43レベルを低減させた。定量的逆転写ポリメラーゼ連鎖反応(qRT-PCR)を実施してTDP-43 mRNAレベルを測定したところ、患者の運動ニューロンにおいて、TDP-43 mRNAレベルが非標的siRNA(siCTRL)に曝露させたものと比較して低減していることが確認された(図86A)。患者の運動ニューロンにおけるTDP-43枯渇が、STMN2完全長転写物の減少及びSTMN2 RNAのトランケート(ミススプライシング)型の強力な誘導を引き起こすことが更に確認された(図86B~86C)。
したがって、これらの結果により、患者のSTMN2がTDP-43により調節されていることが確認された。更に、患者の運動ニューロンにおけるTDP-43レベルの枯渇は、完全長転写物を代償としてトランケートされた潜在性STMN2 mRNA転写物をもたらす、STMN2のミススプライシングを直接引き起こすということが確立された。これらの結果を用いて、患者の運動ニューロンにおける病理学的作用が、アンチセンスオリゴヌクレオチドを使用した治療的調節(ヌシネルセン、エテプリルセン、ミポメルセン、ミラセン、及びジャシフセン(jacifusen)に使用される薬理学的アプローチ)に適用可能であるか否かを更に評価した。
ASOの設計及びスクリーニング
設計したASOが患者の遺伝子シグネチャと適合することを確実にするために、STMN2潜在性エクソンの周辺領域(TDP-43機能不全時に保持されるイントロン領域)を、患者のiPS細胞から抽出したゲノムDNAからPCR増幅した。この領域に焦点を合わせたのは、潜在性スプライス部位から潜在性ポリアデニル化部位までのRNA領域(これにはTDP-43結合部位が含まれる)をASOの標的とすることによって、STMN2転写の欠損をレスキューすることができると仮定したからである。次に、PCR産物のサンガーシーケンシングを行い、標的領域が患者の配列と参照ゲノムとの間で完全に適合することを確認した(図87A、図87C)。
設計したASOが患者の遺伝子シグネチャと適合することを確実にするために、STMN2潜在性エクソンの周辺領域(TDP-43機能不全時に保持されるイントロン領域)を、患者のiPS細胞から抽出したゲノムDNAからPCR増幅した。この領域に焦点を合わせたのは、潜在性スプライス部位から潜在性ポリアデニル化部位までのRNA領域(これにはTDP-43結合部位が含まれる)をASOの標的とすることによって、STMN2転写の欠損をレスキューすることができると仮定したからである。次に、PCR産物のサンガーシーケンシングを行い、標的領域が患者の配列と参照ゲノムとの間で完全に適合することを確認した(図87A、図87C)。
患者の運動ニューロンのSTMN2転写物で観察されたスプライシング欠損の補正を試みるために、この領域を標的とするASOを設計し合成した。特に、構造化されておらず、それによりASOが結合しやすい可能性があると予測されるプレmRNAの領域に相補的であるように、数個のASOを設計した(この領域は、潜在性スプライス部位以降の塩基94~121である)。これらのASOを、2つの異なる化学物質(2’-O-メトキシエチルRNA(MOE)、及びMOEとロックド核酸とのキメラ。全ての配列にホスホロチオエート結合が含まれる)を使用して合成し、潜在性エクソンのちょうど5’から3’ポリアデニル化部位の範囲のイントロンに沿って並べた(図82)。化合物にはDNAが含まれていないため、これらの標的化ASOは転写物に結合し、立体的に作用して適切なSTMN2スプライシングを促進することが予想された。
患者の運動ニューロンにおいて、合計51個のASOを、(1)トランケートされたSTMN2転写物の生成を抑制する能力、及び(2)完全長STMN2転写物を回復させる能力についてスクリーニングした。ASO SJ+94及びASO SJ-1を、患者の運動ニューロンにおいて、STMN2の潜在性スプライシングを抑制し、かつ(2つの異なる実験にて)完全長STMN2 RNAを回復させ、患者の運動ニューロンのSTMN2タンパク質レベルを押し上げ、かつ患者の運動ニューロンの軸索再成長を促進する(すなわち、真の臨床的利益のための可能性を創出する)という能力に基づいて、下記の反復スクリーニング実験後に候補として選択した。
第1の実験では、患者の運動ニューロンをsiTARDBPで処置し、次いで、全RNAを抽出する前に、患者の運動ニューロンをある濃度範囲(30nM~0.03nMの範囲)にわたって様々なASOとともに培養した。抽出したRNAを使用して、逆転写によってcDNAを合成した。RNA18S5発現を使用して正規化した、トランケートされたSTMN2 RNA及び完全長STMN2 RNAの両方のレベルを、qRT-PCRを使用して評価した。多くのASOが有望な結果を示す一方で、ASO SJ+94の結果は際立っていたが、これは、ASO SJ+94が患者の運動ニューロンにおいて非標的化対照ASO-NTCと比較して、用量依存的に(i)潜在性スプライシングを抑制し(図88A)、かつ(ii)完全長STMN2 RNAを回復させる(図88B)ことができたからであった。更に、ASO SJ-1の結果は、患者の運動ニューロンにおいて非標的化対照ASO-NTCと比較して、(i)潜在性スプライシングの抑制(図95A)及び(ii)完全長STMN2 RNAの回復(図95B)において有効かつ安全であった。
ASOの有効性の概要
ASO(SJ+94)及びASO(SJ-1)が、核内TDP-43が低減した場合に、患者の運動ニューロンにおいてSTMN2の潜在性スプライシングを抑制し、完全長STMN2 RNAを回復したことが立証された。次に、TDP-43が誤局在化された場合に、別の実験パラダイムにおいてこのことが有効であると証明されるか否かを評価した。死後組織の試験により、TDP-43の誤局在化及び細胞質におけるその凝集が散発性ALSの特徴であることが示された。いくつかのグループは、散発性ALS患者の死後組織で観察されるものと同類のTDP-43の細胞質凝集が、プロテアソームの薬理学的阻害に応答して生じることを報告している(1、4)。このTDP-43の誤局在化は、STMN2を含むその転写物の発現変化を引き起こすことも示されている。
ASO(SJ+94)及びASO(SJ-1)が、核内TDP-43が低減した場合に、患者の運動ニューロンにおいてSTMN2の潜在性スプライシングを抑制し、完全長STMN2 RNAを回復したことが立証された。次に、TDP-43が誤局在化された場合に、別の実験パラダイムにおいてこのことが有効であると証明されるか否かを評価した。死後組織の試験により、TDP-43の誤局在化及び細胞質におけるその凝集が散発性ALSの特徴であることが示された。いくつかのグループは、散発性ALS患者の死後組織で観察されるものと同類のTDP-43の細胞質凝集が、プロテアソームの薬理学的阻害に応答して生じることを報告している(1、4)。このTDP-43の誤局在化は、STMN2を含むその転写物の発現変化を引き起こすことも示されている。
TDP-43の核内枯渇を誘導する、患者のニューロンにおけるプロテアソーム阻害(MG-132(1uM))は、STMN2の発現低下をもたらした(図89)。実際、ASO SJ+94で処置した患者の運動ニューロンは、非標的化対照ASO(NTC)で処置したものよりも有意に高いレベルの完全長STMN2 RNAを維持した(p値0.0024)(図89)。更に、ASO SJ-1で処置した患者の運動ニューロンは、非標的化対照ASO(NTC)で処置したものよりも有意に高い(30%高い)レベルの完全長STMN2 RNAを維持した(これはp値0.0003に換算される)(図96)。
STMN2 ASOが転写物レベルに影響を及ぼすことができることを立証及び検証した後、STMN2 ASOがTDP-43の低減後に観察されたタンパク質レベルの減少もレスキューすることができるか否かの判定を試みた。患者の運動ニューロンを、siRNAと、非標的化ASO(NTC)またはスクリーニングからのリード化合物のうちの1つのいずれかとで処置した(図90、図97)。陽性対照として、STMN2タンパク質レベルを押し上げることがこれまでに実証されている確立されたJNK阻害剤(JNKi)SP600125とともに、患者の運動ニューロンを培養した(1、5)。その後の免疫ブロット分析により、STMN2タンパク質レベルが、siTDPによる核内TDP-43の喪失後に低下し、JNK阻害後に増加したことが示された(図90)。非標的化対照ASO(NTC)で処置した細胞とは異なり、リード候補物では、siRNA対照のレベルまでSTMN2が回復することが観察された。これらの総合的な結果により、試験したASOが、完全長転写物に有利に働き新生STMN2 RNA転写物のトランケート型へのプロセシングを防止し、タンパク質レベルを正常に回復させることが実証された。
軸索再生に対するASOの有効性の概要
TDP-43の枯渇が損傷後の軸索再成長の低減につながることが過去に実証された(1)。同様の表現型が、STMN2のレベルが低減したか、またはSTMN2が完全に欠如したhMNで観察され、これはSTMN2の回復またはSTMN2の翻訳後安定化によってレスキューすることができた(1、2)。これらの結果は、STMN2をALSで観察される運動ニューロパチーに強く関連付ける。ASO SJ+94がTDP-43枯渇及び損傷後の軸索再成長をレスキューすることができるか否かを試験するために、患者の運動ニューロンを、神経細胞体とは異なるチャンバーへの軸索成長を可能にするマイクロ流体デバイスで培養した(図91A)。デバイスの体細胞区画中で7日間培養したニューロンは、軸索をマイクロチャネルを通して軸索チャンバーへと伸長した。ニューロンをsiTARDBP及びASO SJ+94で処置してから、体細胞区画内の細胞体を妨害することなく軸索を切断した。次に、軸索伸長をマイクロチャネルから測定して、損傷後の再成長を評価した(図91B、図91D)。分析により、非標的化対照ASOと比較して、ASO SJ+94による再成長が有意に増加することが明らかとなった(図91C)。分析により、非標的化対照ASOと比較して、ASO SJ-1による再成長が有意に増加し、平均値がそれぞれ243um及び176um(p値0.0014)であることが更に明らかとなった(図91E)。
TDP-43の枯渇が損傷後の軸索再成長の低減につながることが過去に実証された(1)。同様の表現型が、STMN2のレベルが低減したか、またはSTMN2が完全に欠如したhMNで観察され、これはSTMN2の回復またはSTMN2の翻訳後安定化によってレスキューすることができた(1、2)。これらの結果は、STMN2をALSで観察される運動ニューロパチーに強く関連付ける。ASO SJ+94がTDP-43枯渇及び損傷後の軸索再成長をレスキューすることができるか否かを試験するために、患者の運動ニューロンを、神経細胞体とは異なるチャンバーへの軸索成長を可能にするマイクロ流体デバイスで培養した(図91A)。デバイスの体細胞区画中で7日間培養したニューロンは、軸索をマイクロチャネルを通して軸索チャンバーへと伸長した。ニューロンをsiTARDBP及びASO SJ+94で処置してから、体細胞区画内の細胞体を妨害することなく軸索を切断した。次に、軸索伸長をマイクロチャネルから測定して、損傷後の再成長を評価した(図91B、図91D)。分析により、非標的化対照ASOと比較して、ASO SJ+94による再成長が有意に増加することが明らかとなった(図91C)。分析により、非標的化対照ASOと比較して、ASO SJ-1による再成長が有意に増加し、平均値がそれぞれ243um及び176um(p値0.0014)であることが更に明らかとなった(図91E)。
参照文献
1.Klim JR,Williams LA,Limone F,Guerra San Juan I,Davis-Dusenbery BN,Mordes DA,Burberry A,Steinbaugh MJ,Gamage KK,Kirchner R,Moccia R,Cassel SH,Chen K,Wainger BJ,Woolf CJ,Eggan K.ALS-implicated protein TDP-43 sustains levels of STMN2,a mediator of motor neuron growth and repair.Nat Neurosci.2019;22(2):167-79.Epub 2019/01/16.doi:10.1038/s41593-018-0300-4.PubMed PMID:30643292.
2.Melamed Z,Lopez-Erauskin J,Baughn MW,Zhang O,Drenner K,Sun Y,Freyermuth F,McMahon MA,Beccari MS,Artates JW,Ohkubo T,Rodriguez M,Lin N,Wu D,Bennett CF,Rigo F,Da Cruz S,Ravits J,Lagier-Tourenne C,Cleveland DW.Premature polyadenylation-mediated loss of stathmin-2 is a hallmark of TDP-43-dependent neurodegeneration.Nat Neurosci.2019;22(2):180-90.Epub 2019/01/16.doi: 10.1038/s41593-018-0293-z.PubMed PMID:30643298;PMCID:PMC6348009.
3.Prudencio M,Humphrey J,Pickles S,Brown AL,Hill SE,Kachergus J,Shi J,Heckman M,Spiegel M,Cook C,Song Y,Yue M,Daughrity L,Carlomagno Y,Jansen-West K,Fernandez De Castro C,DeTure M,Koga S,Wang YC,Sivakumar P,Bodo C,Candalija A,Talbot K,Selvaraj BT,Burr K,Chandran S,Newcombe J,Lashley T,Hubbard I,Catalano D,Kim D,Propp N,Fennessey S,Fagegaltier D,Phatnani H,Secrier M,Fisher EM,Oskarsson B,van Blitterswijk M,Rademakers R,Graff-Radford NR,Boeve B,Knopman DS,Petersen R,Josephs K,Thompson EA,Raj T,Ward ME,Dickson D,Gendron TF,Fratta P,Petrucelli L.Truncated stathmin-2 is a marker of TDP-43 pathology in frontotemporal dementia.J Clin Invest.2020.Epub 2020/08/14.doi:10.1172/JCI139741.PubMed PMID:32790644.
4.van Eersel J,Ke YD,Gladbach A,Bi M,Gotz J,Kril JJ,Ittner LM.Cytoplasmic accumulation and aggregation of TDP-43 upon proteasome inhibition in cultured neurons.PLoS One.2011;6(7):e22850.Epub 2011/08/11.doi:10.1371/journal.pone.0022850.PubMed PMID:21829535;PMCID:PMC3146516.
5.Shin JE,Miller BR,Babetto E,Cho Y,Sasaki Y,Qayum S,Russler EV,Cavalli V,Milbrandt J,DiAntonio A.SCG10 is a JNK target in the axonal degeneration pathway.Proc Natl Acad Sci U S A.2012;109(52):E3696-705.Epub 2012/11/29.doi:10.1073/pnas.1216204109.PubMed PMID:23188802;PMCID:PMC3535671.
1.Klim JR,Williams LA,Limone F,Guerra San Juan I,Davis-Dusenbery BN,Mordes DA,Burberry A,Steinbaugh MJ,Gamage KK,Kirchner R,Moccia R,Cassel SH,Chen K,Wainger BJ,Woolf CJ,Eggan K.ALS-implicated protein TDP-43 sustains levels of STMN2,a mediator of motor neuron growth and repair.Nat Neurosci.2019;22(2):167-79.Epub 2019/01/16.doi:10.1038/s41593-018-0300-4.PubMed PMID:30643292.
2.Melamed Z,Lopez-Erauskin J,Baughn MW,Zhang O,Drenner K,Sun Y,Freyermuth F,McMahon MA,Beccari MS,Artates JW,Ohkubo T,Rodriguez M,Lin N,Wu D,Bennett CF,Rigo F,Da Cruz S,Ravits J,Lagier-Tourenne C,Cleveland DW.Premature polyadenylation-mediated loss of stathmin-2 is a hallmark of TDP-43-dependent neurodegeneration.Nat Neurosci.2019;22(2):180-90.Epub 2019/01/16.doi: 10.1038/s41593-018-0293-z.PubMed PMID:30643298;PMCID:PMC6348009.
3.Prudencio M,Humphrey J,Pickles S,Brown AL,Hill SE,Kachergus J,Shi J,Heckman M,Spiegel M,Cook C,Song Y,Yue M,Daughrity L,Carlomagno Y,Jansen-West K,Fernandez De Castro C,DeTure M,Koga S,Wang YC,Sivakumar P,Bodo C,Candalija A,Talbot K,Selvaraj BT,Burr K,Chandran S,Newcombe J,Lashley T,Hubbard I,Catalano D,Kim D,Propp N,Fennessey S,Fagegaltier D,Phatnani H,Secrier M,Fisher EM,Oskarsson B,van Blitterswijk M,Rademakers R,Graff-Radford NR,Boeve B,Knopman DS,Petersen R,Josephs K,Thompson EA,Raj T,Ward ME,Dickson D,Gendron TF,Fratta P,Petrucelli L.Truncated stathmin-2 is a marker of TDP-43 pathology in frontotemporal dementia.J Clin Invest.2020.Epub 2020/08/14.doi:10.1172/JCI139741.PubMed PMID:32790644.
4.van Eersel J,Ke YD,Gladbach A,Bi M,Gotz J,Kril JJ,Ittner LM.Cytoplasmic accumulation and aggregation of TDP-43 upon proteasome inhibition in cultured neurons.PLoS One.2011;6(7):e22850.Epub 2011/08/11.doi:10.1371/journal.pone.0022850.PubMed PMID:21829535;PMCID:PMC3146516.
5.Shin JE,Miller BR,Babetto E,Cho Y,Sasaki Y,Qayum S,Russler EV,Cavalli V,Milbrandt J,DiAntonio A.SCG10 is a JNK target in the axonal degeneration pathway.Proc Natl Acad Sci U S A.2012;109(52):E3696-705.Epub 2012/11/29.doi:10.1073/pnas.1216204109.PubMed PMID:23188802;PMCID:PMC3535671.
当業者は、単なる通常の実験を使用して、本明細書に記載される特定の実施形態に対する多くの等価物を認識するか、または確認することができるであろう。本発明の範囲は、発明を実施するための形態またはその中に記載される詳細に限定されることを意図するものではない。「a」、「an」、及び「the」などの冠詞は、その反対が示されるか、または別途文脈から明らかでない限り、1つまたは2つ以上を意味し得る。群の1つ以上の要素の間に「または」または「及び/または」を含む請求項または説明は、その反対が示されるか、または別途文脈から明らかでない限り、1つ、2つ以上、または全ての群要素が、所与の製品またはプロセスにおいて存在するか、用いられるか、またはそれらに別途関連している場合に、満たされると考えられる。本発明は、群の正確に1つの要素が、所与の製品またはプロセスにおいて存在するか、用いられるか、またはそれらに別途関連している実施形態を含む。本発明は、2つ以上、または全ての群要素が、所与の製品またはプロセスにおいて存在するか、用いられるか、またはそれらに別途関連している実施形態を含む。更に、本発明は、請求項(当初の請求項であるかまたは後に追加された請求項であるかを問わない)のうちの1項以上からの1つ以上の制限、要素、条項、記述用語などが、別の請求項(当初のものであるかまたは後に追加されたものであるかを問わない)に導入される全ての変形、組み合わせ、及び順列を包含することを理解されたい。例えば、別の請求項に従属する任意の請求項は、任意の他の請求項、例えば、同一の基本請求項に従属する任意の他の請求項に見出される1つ以上の要素(複数可)、特徴(複数可)または制限(複数可)を含むように修正され得る。任意の1項以上の請求項を修正して、任意の1つ以上の実施形態(複数可)、要素(複数可)、特徴(複数可)などを明示的に除外することができる。例えば、任意の特定のシデロフレキシン(sideroflexin)、シデロフレキシンモジュレーター、細胞タイプ、がんタイプなどを、任意の1項以上の請求項から除外することができる。
(i)任意の分類方法、予測方法、処置選択方法、処置方法などは、試料、例えば、がんに関する分類、予測、処置選択、処置を必要とする対象から得られた試料、例えば、対象から得られたがん試料を提供するステップを含み得ること;(ii)任意の分類方法、予測方法、処置選択方法、処置方法などは、がんに関するそのような分類、予測、処置選択、または処置を、それを必要とする対象に提供するステップを含み得ることが理解されるべきである。
請求項が方法を記載している場合、本発明の特定の態様は、その方法を実施するのに適した製品、例えば、キット、薬剤、または組成物を提供する。
要素が、リストとして、例えば、マーカッシュ群形式で提示される場合、要素の各亜群も開示され、任意の要素(複数可)をこの群から除去することができる。簡潔にするためにこれらの実施形態のいくつかのみが本明細書に具体的に記載されているが、本開示は、そのような全ての実施形態を包含する。一般的に、本発明、または本発明の態様が特定の要素、特徴などを含むように言及される場合、本発明の特定の実施形態または本発明の態様が、そのような要素、特徴などからなるか、または本質的になることもまた、理解されるべきである。
本明細書で数値範囲が言及される場合、本発明は、端点が含まれる実施形態、両方の端点が除外される実施形態、及び一方の端点が含まれ、他方が除外される実施形態を含む。別途示されていない限り、両方の端点が含まれていると想定されるべきである。更に、別途示されるか、または別途文脈及び当業者の理解から明らかでない限り、範囲として表される値は、文脈上別途明確に示されない限り、その範囲の下限の単位の10分の1まで、本発明の異なる実施形態の記載範囲内の任意の適正な値または部分範囲をとることができる。「X未満」、「Xより大きい」、または「少なくともX」などの語句が使用される場合(Xは数またはパーセンテージである)、任意の合理的な値が範囲の下限または上限として選択され得ることが理解されるべきである。数値のリストが本明細書に記載される場合(「少なくとも」で始まるか否かを問わない)、本発明は、リスト中の任意の2つの値によって定義される任意の介在値または範囲に関連する実施形態を含み、最も低い値を最小値と見なすことができ、最も大きな値を最大値と見なすことができることもまた、理解されるべきである。更に、パーセンテージなどの数のリストが「少なくとも」で始まる場合、この用語はリスト内の各数に適用される。数値が「約」または「およそ」で始まる本発明の任意の実施形態について、本発明は、厳密な値が記載されている実施形態を含む。数値が「約」または「およそ」で始まらない本発明の任意の実施形態について、本発明は、値が「約」または「およそ」で始まる実施形態を含む。「およそ」または「約」は、別途記載のない限りまたは別途文脈から明らか(例えば、そのような数が考えられる値の100%を許容できないほど超える場合)でない限り、一般に、いずれかの方向(その数よりも大きいかまたは小さい)の数の1%、またはいくつかの実施形態では5%、またはいくつかの実施形態では10%の範囲内にある数を含む。
反対のことが明確に示されない限り、2つ以上の行為を含む、本明細書で特許請求される任意の方法において、方法の行為の順序は、方法の行為が記載された順序に必ずしも限定されないが、本開示は、順序がそのように限定される実施形態を包含することが理解されるべきである。いくつかの実施形態では、方法は、個人または実体によって実施され得る。いくつかの実施形態では、方法のステップは、方法が集合的に実施されるように、2人以上の個人または2つ以上の実体によって実施され得る。いくつかの実施形態では、方法は、方法の1つ、2つ以上、または全てのステップを実施するように別の個人または実体に要求または許可することによって、少なくとも部分的に実施され得る。いくつかの実施形態では、方法は、2つ以上の実体または2人以上の個人に、それぞれが方法の少なくとも1つのステップを実施するように要求することを含む。いくつかの実施形態では、2つ以上のステップの実施は、方法が集合的に実施されるように調整される。別途示さない限り、または文脈から明らかでない限り、本明細書に記載の任意の製品または組成物が、「単離されている」と見なされ得ることも理解されるべきである。適用可能な場合、別途示さない限りまたは文脈から明らかでない限り、精神的に、または精神的ステップとして実施するか、またはペンもしくは鉛筆などの筆記用具及び紙などの筆記に適した表面を使用して実施するのに適し得る方法の任意の方法またはステップは、機械、例えば、コンピュータ、デバイス(装置)、またはシステムによって、少なくとも部分的に、実質的に、または全体的に実施されるものとして明示的に示すことができ、これは、いくつかの実施形態では、そのような方法もしくはステップまたはそれらの一部を実施することができるように特別に適合または設計され得ることもまた、理解されるべきである。
本明細書で使用されるセクション見出しは、いかなる意味においても限定するものであると解釈されるべきではない。任意のセクション見出しの下に提示される主題は、本明細書に記載の任意の態様または実施形態に適用可能であり得ることが明確に企図される。
本明細書の実施形態または態様は、本明細書に記載の任意の薬剤、組成物、物品、キット、及び/または方法に関し得る。任意の1つ以上の実施形態または態様は、適切な場合は常に、任意の1つ以上の他の実施形態または態様と自由に組み合わせることができることが企図される。例えば、相互に矛盾しない2つ以上の薬剤、組成物、物品、キット、及び/または方法の任意の組み合わせが提供される。本明細書における任意の場所の用語に関する任意の説明または例示は、別途示されないかまたは明白に明らかでない限り、そのような用語が本明細書中に現れる場合は常に(例えば、そのような用語が関連する任意の態様または実施形態において)適用され得ることが理解されよう。
Claims (121)
- STMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、STMN2タンパク質発現を増加させる、アンチセンスオリゴヌクレオチド。
- STMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、それにより不完全なまたは変化したSTMN2 RNA配列の包含を抑制または防止するアンチセンスオリゴヌクレオチドであって、
前記STMN2 RNA配列のポリアデニル化部位に結合しない、前記アンチセンスオリゴヌクレオチド。 - 不完全なまたは変化したSTMN2 RNA配列が、TDP-43の機能が減退しているかまたはTDP病変が存在する場合に発生しかつ存在量が増加する、請求項1に記載のアンチセンスオリゴヌクレオチド。
- 潜在性エクソンをコードするSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、それによりSTMN2 RNAへの潜在性エクソンの包含を抑制または防止するアンチセンスオリゴヌクレオチドであって、
前記STMN2 mRNA配列、プレmRNA配列、または新生RNA配列のポリアデニル化部位に結合しない、前記アンチセンスオリゴヌクレオチド。 - 5’スプライス部位、3’スプライス部位、または通常のTDP-43結合部位を標的とするように設計されている、請求項1~4のいずれか1項に記載のアンチセンスオリゴヌクレオチド。
- 一本鎖領域を標的とするように設計されている、請求項1~4のいずれか1項に記載のアンチセンスオリゴヌクレオチド。
- TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とするように設計されている、請求項6に記載のアンチセンスオリゴヌクレオチド。
- 1つ以上のスプライス部位を標的とする、請求項1~7のいずれか1項に記載のアンチセンスオリゴヌクレオチド。
- 配列番号37~85からなる群から選択される配列を含む、アンチセンスオリゴヌクレオチド。
- 配列番号37~74からなる群から選択される配列を含む、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含む、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 配列番号52を含む、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含む、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 配列番号73を含む、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 配列番号53を含む、請求項9に記載のアンチセンスオリゴヌクレオチド。
- STMN2 RNAへの潜在性エクソンの包含を抑制または防止する、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 潜在性エクソンをコードするSTMN2 RNA配列、プレmRNA配列、または新生RNA配列に特異的に結合する、請求項9に記載のアンチセンスオリゴヌクレオチド。
- STMN2タンパク質を増加させる、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 5’スプライス部位、3’スプライス部位、または通常のTDP-43結合部位を標的とするように設計されている、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 潜在性スプライス部位の近位部位、早期ポリアデニル化部位の近位部位、または潜在性スプライス部位と早期ポリアデニル化部位との間に位置する部位を標的とするように設計されている、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 一本鎖領域を標的とするように設計されている、請求項9に記載のアンチセンスオリゴヌクレオチド。
- TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とするように設計されている、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 構造化されていない潜在性エクソン内の標的領域に結合する、請求項9に記載のアンチセンスオリゴヌクレオチド。
- TDP-43により調節される5’スプライス部位の近傍にまたはそれに隣接して結合する、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 予測されるTDP-43結合部位の近位領域を標的とする、請求項9に記載のアンチセンスオリゴヌクレオチド。
- TDP-43の通常の結合部位を標的とする、請求項9に記載のアンチセンスオリゴヌクレオチド。
- 配列番号37~85からなる群から選択される配列を含む1つ以上のアンチセンスオリゴヌクレオチドを含む、医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号37~74からなる群から選択される配列を含む、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含む、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号52を含む、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含む、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号73を含む、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号53を含む、請求項27に記載の医薬組成物。
- 前記組成物が、2つ以上のアンチセンスオリゴヌクレオチドを含む、請求項27に記載の医薬組成物。
- 前記2つ以上のアンチセンスオリゴヌクレオチドが、共有結合されている、請求項27に記載の医薬組成物。
- 前記組成物が、3つ以上のアンチセンスオリゴヌクレオチドを含む、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、STMN2タンパク質発現を増加させる、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、5’スプライス部位、3’スプライス部位、または通常のTDP-43結合部位を標的とするように設計されている、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、潜在性スプライス部位の近位部位、早期ポリアデニル化部位の近位部位、または潜在性スプライス部位と早期ポリアデニル化部位との間に位置する部位を標的とするように設計されている、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、一本鎖領域を標的とするように設計されている、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とするように設計されている、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、構造化されていない潜在性エクソン内の標的領域に結合する、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、TDP-43により調節される5’スプライス部位の近傍にまたはそれに隣接して結合する、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、予測されるTDP-43結合部位の近位領域を標的とする、請求項27に記載の医薬組成物。
- 前記アンチセンスオリゴヌクレオチドが、TDP-43の通常の結合部位を標的とする、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、1つ以上のスプライス部位を標的とする、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、STMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合し、それにより不完全なまたは変化したSTMN2 RNA配列の包含を抑制または防止する、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、潜在性エクソンをコードするSTMN2 mRNA配列、プレmRNA配列、または新生RNA配列に特異的に結合する、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、STMN2 RNAへの潜在性エクソンの包含を抑制または防止する、請求項27に記載の医薬組成物。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、潜在性スプライシングを抑制する、請求項27に記載の医薬組成物。
- 神経変性疾患を処置するための薬剤を更に含む、請求項27に記載の医薬組成物。
- 外傷性脳損傷を処置するための薬剤を更に含む、請求項27に記載の医薬組成物。
- プロテアソーム阻害剤誘導性ニューロパチーを処置するための薬剤を更に含む、請求項27に記載の医薬組成物。
- 遺伝子治療薬としてSTMN2を更に含む、請求項27に記載の医薬組成物。
- JNK阻害剤を更に含む、請求項27に記載の医薬組成物。
- 配列番号37~85からなる群から選択される1つ以上の配列を含む多量体オリゴヌクレオチドを含む、医薬組成物。
- 前記多量体オリゴヌクレオチドが、配列番号37~85からなる群から選択される2つ以上の配列を含む、請求項56に記載の医薬組成物。
- TAR DNA結合タンパク質43(TDP-43)の機能性の減退に関連する疾患もしくは状態を処置すること、または前記疾患もしくは状態の可能性を低減させることを必要とする対象の神経細胞における、前記疾患もしくは状態を処置するか、または前記疾患もしくは状態の可能性を低減させる方法であって、
STMN2タンパク質のレベルの低減を補正するアンチセンスオリゴヌクレオチドに前記神経細胞を接触させることを含み、薬剤が、標的転写物のポリアデニル化部位を標的としない、前記方法。 - TAR DNA結合タンパク質43(TDP-43)の機能性の減退に関連する疾患もしくは状態を処置すること、または前記疾患もしくは状態の可能性を低減させることを必要とする対象の神経細胞における、前記疾患もしくは状態を処置するか、または前記疾患もしくは状態の可能性を低減させる方法であって、
STMN2タンパク質発現を増加させるアンチセンスオリゴヌクレオチドに前記神経細胞を接触させることを含む、前記方法。 - 前記アンチセンスオリゴヌクレオチドが、潜在性エクソンをコードするSTMN2 RNA配列、プレRNA配列、または新生RNA配列に特異的に結合する、請求項59に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、5’スプライス部位、3’スプライス部位、または通常のTDP-43結合部位を標的とするように設計されている、請求項59に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、潜在性スプライス部位の近位部位、早期ポリアデニル化部位の近位部位、または潜在性スプライス部位と早期ポリアデニル化部位との間に位置する部位を標的とするように設計されている、請求項59に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、一本鎖領域を標的とするように設計されている、請求項59に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とするように設計されている、請求項59に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、構造化されていない潜在性エクソン内の標的領域に結合する、請求項59に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、TDP-43により調節される5’スプライス部位の近傍にまたはそれに隣接して結合する、請求項59に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、予測されるTDP-43結合部位の近位領域を標的とする、請求項59に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、1つ以上のスプライス部位を標的とするように設計されている、請求項59に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、正常長のまたはタンパク質をコードするSTMN2プレmRNAまたはmRNAを回復させる、請求項59に記載の方法。
- 前記対象が、ニューロンの成長及び修復の改善を示す、請求項59に記載の方法。
- 前記疾患または状態が、神経変性疾患である、請求項59に記載の方法。
- 前記疾患または状態が、筋萎縮性側索硬化症(ALS)、前頭側頭型認知症(FTD)、封入体筋炎(IBM)、パーキンソン病、及びアルツハイマー病からなる群から選択される、請求項59に記載の方法。
- 前記疾患または状態が、外傷性脳損傷である、請求項59に記載の方法。
- 前記疾患または状態が、プロテアソーム阻害剤誘導性ニューロパチーである、請求項59に記載の方法。
- 前記疾患または状態が、神経細胞におけるTDP-43のレベルの変異または低減に関連する、請求項59に記載の方法。
- 有効量の第2の薬剤を前記対象に投与することを更に含む、請求項59に記載の方法。
- 前記第2の薬剤が、神経変性疾患を処置するために投与される、請求項76に記載の方法。
- 前記第2の薬剤が、外傷性脳損傷を処置するために投与される、請求項76に記載の方法。
- 前記第2の薬剤が、遺伝子治療薬として投与されるSTMN2である、請求項76に記載の方法。
- TAR DNA結合タンパク質43(TDP-43)の機能性の減退に関連する疾患もしくは状態を処置するか、または前記疾患もしくは前記状態の可能性を低減させることを必要とする対象の神経細胞における、前記疾患もしくは前記状態を処置するか、または前記疾患もしくは前記状態の可能性を低減させる方法であって、
STMN2タンパク質のレベルの低減を補正する1つ以上のアンチセンスオリゴヌクレオチドに前記神経細胞を接触させることを含み、前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号37~85からなる群から選択される配列を含む、前記方法。 - 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号37~74からなる群から選択される配列を含む、請求項80に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含む、請求項80に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号52を含む、請求項80に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含む、請求項80に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号73を含む、請求項80に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号53を含む、請求項80に記載の方法。
- TAR DNA結合タンパク質43(TDP-43)の機能性の減退に関連する疾患もしくは状態を処置するか、または前記疾患もしくは前記状態の可能性を低減させることを必要とする対象の神経細胞における、前記疾患もしくは前記状態を処置するか、または前記疾患もしくは前記状態の可能性を低減させる方法であって、
STMN2 RNAへの潜在性エクソンの包含を抑制または防止する1つ以上のアンチセンスオリゴヌクレオチドに前記神経細胞を接触させることを含み、前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号37~85からなる群から選択される配列を含む、前記方法。 - 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号37~74からなる群から選択される配列を含む、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号40、配列番号47、配列番号48、配列番号49、配列番号50、配列番号52、配列番号53、配列番号54、配列番号56、及び配列番号78からなる群から選択される配列を含む、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号52を含む、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号53、配列番号72、及び配列番号73からなる群から選択される配列を含む、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号73を含む、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、配列番号53を含む、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、潜在性エクソンをコードするSTMN2 RNA配列、プレRNA配列、または新生RNA配列に特異的に結合する、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、5’スプライス部位、3’スプライス部位、または通常のTDP-43結合部位を標的とするように設計されている、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、潜在性スプライス部位の近位部位、早期ポリアデニル化部位の近位部位、または潜在性スプライス部位と早期ポリアデニル化部位との間に位置する部位を標的とするように設計されている、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、一本鎖領域を標的とするように設計されている、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、TDP-43結合部位とポリアデニル化部位との間に位置する一本鎖領域を標的とするように設計されている、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、構造化されていない前記潜在性エクソン内の標的領域に結合する、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、TDP-43により調節される5’スプライス部位の近傍にまたはそれに隣接して結合する、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、予測されるTDP-43結合部位の近位領域を標的とする、請求項87に記載の方法。
- 前記1つ以上のアンチセンスオリゴヌクレオチドが、TDP-43の通常の結合部位を標的とする、請求項87に記載の方法。
- 前記疾患または状態が、筋萎縮性側索硬化症(ALS)、前頭側頭型認知症(FTD)、封入体筋炎(IBM)、パーキンソン病、及びアルツハイマー病からなる群から選択される、請求項87に記載の方法。
- 前記疾患または状態が、外傷性脳損傷である、請求項87に記載の方法。
- 前記疾患または状態が、プロテアソーム阻害剤誘導性ニューロパチーである、請求項87に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、潜在性スプライシングを抑制する、請求項87に記載の方法。
- 前記アンチセンスオリゴヌクレオチドが、STMN2タンパク質発現を増加させる、請求項87に記載の方法。
- 前記対象が、ニューロンの成長及び修復の改善を示す、請求項87に記載の方法。
- 有効量の第2の薬剤を前記対象に投与することを更に含む、請求項87に記載の方法。
- 前記第2の薬剤が、神経変性疾患を処置するために投与される、請求項109に記載の方法。
- 前記第2の薬剤が、外傷性脳損傷を処置するために投与される、請求項109に記載の方法。
- TAR DNA結合タンパク質43(TDP-43)の機能性の減退に関連する疾患もしくは状態を処置するか、または前記疾患もしくは前記状態の可能性を低減させることを必要とする対象の神経細胞における、前記疾患もしくは前記状態を処置するか、または前記疾患もしくは前記状態の可能性を低減させる方法であって、
STMN2タンパク質のレベルの低減を補正する多量体オリゴヌクレオチドに前記神経細胞を接触させることを含み、前記多量体オリゴヌクレオチドが、配列番号37~85からなる群から選択される2つ以上のアンチセンスオリゴヌクレオチドを含む、前記方法。 - 前記多量体オリゴヌクレオチドが、配列番号37~74からなる群から選択される2つ以上のアンチセンスオリゴヌクレオチドを含む、請求項112に記載の方法。
- STMN2タンパク質のレベルの低減を補正するアンチセンスオリゴヌクレオチドであって、
潜在性エクソン内の非構造化領域を標的とするように設計されている、前記アンチセンスオリゴヌクレオチド。 - 前記潜在性エクソン内の前記非構造化領域が、潜在性スプライス部位と早期ポリアデニル化部位との間に位置する、請求項114に記載のアンチセンスオリゴヌクレオチド。
- 対象におけるSTMN2またはELAVL3タンパク質のレベルの変化を検出する方法であって、
前記対象から試料を得ることと;
前記STMN2またはELAVL3タンパク質のレベルが変化しているか否かを検出することと、を含む、前記方法。 - 前記対象が、筋萎縮性側索硬化症を有する、請求項116に記載の方法。
- 前記対象が、外傷性脳損傷を有する、請求項116に記載の方法。
- 前記STMN2またはELAVL3のレベルが変化しているか否かを検出することが、参照試料と比較して前記STMN2またはELAVL3のレベルが低下しているか否かを判定することを含む、請求項116~118のいずれか1項に記載の方法。
- 前記STMN2またはELAVL3のレベルが変化しているか否かを検出することが、ELISAを使用することを含む、請求項113~119のいずれか1項に記載の方法。
- 前記試料が、生体液試料である、請求項113~120のいずれか1項に記載の方法。
Applications Claiming Priority (7)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| US202062994797P | 2020-03-25 | 2020-03-25 | |
| US62/994,797 | 2020-03-25 | ||
| US202063063174P | 2020-08-07 | 2020-08-07 | |
| US63/063,174 | 2020-08-07 | ||
| US202163133749P | 2021-01-04 | 2021-01-04 | |
| US63/133,749 | 2021-01-04 | ||
| PCT/US2021/024254 WO2021195446A2 (en) | 2020-03-25 | 2021-03-25 | Methods and compositions for restoring stmn2 levels |
Publications (2)
| Publication Number | Publication Date |
|---|---|
| JP2023519871A true JP2023519871A (ja) | 2023-05-15 |
| JPWO2021195446A5 JPWO2021195446A5 (ja) | 2024-04-03 |
Family
ID=77892458
Family Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2022558277A Pending JP2023519871A (ja) | 2020-03-25 | 2021-03-25 | Stmn2レベルを回復させるための方法及び組成物 |
Country Status (6)
| Country | Link |
|---|---|
| US (1) | US20240011027A1 (ja) |
| EP (1) | EP4127172A2 (ja) |
| JP (1) | JP2023519871A (ja) |
| CN (1) | CN116034161A (ja) |
| CA (1) | CA3176884A1 (ja) |
| WO (1) | WO2021195446A2 (ja) |
Families Citing this family (4)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| CA3142526A1 (en) * | 2019-06-03 | 2020-12-10 | Quralis Corporation | Oligonucleotides and methods of use for treating neurological diseases |
| WO2022018187A1 (en) * | 2020-07-23 | 2022-01-27 | F. Hoffmann-La Roche Ag | Oligonucleotides targeting rna binding protein sites |
| GB2617565A (en) * | 2022-04-11 | 2023-10-18 | Ucl Business Ltd | A construct, vector and system and uses thereof |
| GB202208387D0 (en) * | 2022-06-08 | 2022-07-20 | Ucl Business Ltd | Modified U7 snRNA construct |
Family Cites Families (1)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| CA3103429A1 (en) * | 2018-06-14 | 2019-12-19 | Don W. Cleveland | Compounds and methods for increasing stmn2 expression |
-
2021
- 2021-03-25 JP JP2022558277A patent/JP2023519871A/ja active Pending
- 2021-03-25 CA CA3176884A patent/CA3176884A1/en active Pending
- 2021-03-25 WO PCT/US2021/024254 patent/WO2021195446A2/en unknown
- 2021-03-25 EP EP21775261.7A patent/EP4127172A2/en active Pending
- 2021-03-25 CN CN202180040347.7A patent/CN116034161A/zh active Pending
- 2021-03-25 US US17/914,706 patent/US20240011027A1/en active Pending
Also Published As
| Publication number | Publication date |
|---|---|
| US20240011027A1 (en) | 2024-01-11 |
| EP4127172A2 (en) | 2023-02-08 |
| WO2021195446A3 (en) | 2021-11-11 |
| CN116034161A (zh) | 2023-04-28 |
| CA3176884A1 (en) | 2021-09-30 |
| WO2021195446A2 (en) | 2021-09-30 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| Klim et al. | ALS-implicated protein TDP-43 sustains levels of STMN2, a mediator of motor neuron growth and repair | |
| US20220133848A1 (en) | Methods and compositions for restoring stmn2 levels | |
| Ma et al. | γCaMKII shuttles Ca2+/CaM to the nucleus to trigger CREB phosphorylation and gene expression | |
| US20240011027A1 (en) | Methods and compositions for restoring stmn2 levels | |
| Maldifassi et al. | A new IRAK-M-mediated mechanism implicated in the anti-inflammatory effect of nicotine via α7 nicotinic receptors in human macrophages | |
| Chi et al. | The sphingosine 1-phosphate receptor, S1PR1, plays a prominent but not exclusive role in enhancing the excitability of sensory neurons | |
| US20130266588A1 (en) | Agents, Compositions, And Methods For Treating Pruritis And Related Skin Conditions | |
| Feng et al. | Sonic hedgehog is a regulator of extracellular glutamate levels and epilepsy | |
| Gross et al. | Loss of slug compromises DNA damage repair and accelerates stem cell aging in mammary epithelium | |
| JP2021520200A (ja) | 非神経細胞のニューロンへの再プログラミング、及び神経変性疾患または障害を治療するための方法と組成物 | |
| CN116687969A (zh) | 用于治疗衰老相关的损伤的方法和组合物 | |
| Huang et al. | Compression‐induced senescence of nucleus pulposus cells by promoting mitophagy activation via the PINK1/PARKIN pathway | |
| JP2018052908A (ja) | テトラスパニン−2を利用した糖尿病の予防又は治療用組成物と糖尿病治療剤スクリーニング方法(Composition for preventing or treating diabetes and method for screening antidiabetic agents using tetraspanin−2) | |
| Zhao et al. | MiR‐505 promotes M2 polarization in choroidal neovascularization model mice by targeting transmembrane protein 229B | |
| DK2733205T3 (en) | Corticospinal upper motor neurons, methods and compositions for differentiating neural stem cells by modulating CB1 cannabinoid receptor signaling and applications thereof | |
| JP6519851B2 (ja) | 眼細胞の分化マーカーおよび分化制御 | |
| Han et al. | Isoproterenol-induced hypertrophy of neonatal cardiac myocytes and H9c2 cell is dependent on TRPC3-regulated CaV1. 2 expression | |
| Qian et al. | MicroRNA-31 inhibits traumatic brain injury-triggered neuronal cell apoptosis by regulating hypoxia-inducible factor-1A/vascular endothelial growth factor A axis | |
| Reynolds et al. | Proteomic analysis after status epilepticus identifies UCHL1 as protective against hippocampal injury | |
| US11946046B2 (en) | Staufen1 regulating agents and associated methods | |
| US20230190887A1 (en) | Targeting g3bp aggregation to prevent neurodegeneration | |
| Notaras et al. | Compartmentalized nonsense‐mediated mRNA decay regulates synaptic plasticity and cognitive function via GluR1 signaling | |
| Xie | Characterization of Autism Spectrum Disorder-Associated Protein, PTCHD1 | |
| Liu | The study of Murine double minute-2 (Mdm2) in regulating neuronal activity-dependent protein translation | |
| Hinds | Investigation of Novel Factors Governing the Activities of Oncogenic MYC |
Legal Events
| Date | Code | Title | Description |
|---|---|---|---|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20240322 |
|
| A621 | Written request for application examination |
Free format text: JAPANESE INTERMEDIATE CODE: A621 Effective date: 20240322 |