JP2022535452A - 抗原結合タンパク質構築物およびその使用 - Google Patents
抗原結合タンパク質構築物およびその使用 Download PDFInfo
- Publication number
- JP2022535452A JP2022535452A JP2021572559A JP2021572559A JP2022535452A JP 2022535452 A JP2022535452 A JP 2022535452A JP 2021572559 A JP2021572559 A JP 2021572559A JP 2021572559 A JP2021572559 A JP 2021572559A JP 2022535452 A JP2022535452 A JP 2022535452A
- Authority
- JP
- Japan
- Prior art keywords
- seq
- chain variable
- variable domain
- heavy chain
- light chain
- Prior art date
- Legal status (The legal status is an assumption and is not a legal conclusion. Google has not performed a legal analysis and makes no representation as to the accuracy of the status listed.)
- Pending
Links
Images
Classifications
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K51/00—Preparations containing radioactive substances for use in therapy or testing in vivo
- A61K51/02—Preparations containing radioactive substances for use in therapy or testing in vivo characterised by the carrier, i.e. characterised by the agent or material covalently linked or complexing the radioactive nucleus
- A61K51/04—Organic compounds
- A61K51/08—Peptides, e.g. proteins, carriers being peptides, polyamino acids, proteins
- A61K51/10—Antibodies or immunoglobulins; Fragments thereof, the carrier being an antibody, an immunoglobulin or a fragment thereof, e.g. a camelised human single domain antibody or the Fc fragment of an antibody
- A61K51/1018—Antibodies or immunoglobulins; Fragments thereof, the carrier being an antibody, an immunoglobulin or a fragment thereof, e.g. a camelised human single domain antibody or the Fc fragment of an antibody against material from animals or humans
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K16/00—Immunoglobulins [IGs], e.g. monoclonal or polyclonal antibodies
- C07K16/18—Immunoglobulins [IGs], e.g. monoclonal or polyclonal antibodies against material from animals or humans
- C07K16/28—Immunoglobulins [IGs], e.g. monoclonal or polyclonal antibodies against material from animals or humans against receptors, cell surface antigens or cell surface determinants
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K47/00—Medicinal preparations characterised by the non-active ingredients used, e.g. carriers or inert additives; Targeting or modifying agents chemically bound to the active ingredient
- A61K47/50—Medicinal preparations characterised by the non-active ingredients used, e.g. carriers or inert additives; Targeting or modifying agents chemically bound to the active ingredient the non-active ingredient being chemically bound to the active ingredient, e.g. polymer-drug conjugates
- A61K47/51—Medicinal preparations characterised by the non-active ingredients used, e.g. carriers or inert additives; Targeting or modifying agents chemically bound to the active ingredient the non-active ingredient being chemically bound to the active ingredient, e.g. polymer-drug conjugates the non-active ingredient being a modifying agent
- A61K47/68—Medicinal preparations characterised by the non-active ingredients used, e.g. carriers or inert additives; Targeting or modifying agents chemically bound to the active ingredient the non-active ingredient being chemically bound to the active ingredient, e.g. polymer-drug conjugates the non-active ingredient being a modifying agent the modifying agent being an antibody, an immunoglobulin or a fragment thereof, e.g. an Fc-fragment
- A61K47/6835—Medicinal preparations characterised by the non-active ingredients used, e.g. carriers or inert additives; Targeting or modifying agents chemically bound to the active ingredient the non-active ingredient being chemically bound to the active ingredient, e.g. polymer-drug conjugates the non-active ingredient being a modifying agent the modifying agent being an antibody, an immunoglobulin or a fragment thereof, e.g. an Fc-fragment the modifying agent being an antibody or an immunoglobulin bearing at least one antigen-binding site
- A61K47/6843—Medicinal preparations characterised by the non-active ingredients used, e.g. carriers or inert additives; Targeting or modifying agents chemically bound to the active ingredient the non-active ingredient being chemically bound to the active ingredient, e.g. polymer-drug conjugates the non-active ingredient being a modifying agent the modifying agent being an antibody, an immunoglobulin or a fragment thereof, e.g. an Fc-fragment the modifying agent being an antibody or an immunoglobulin bearing at least one antigen-binding site the antibody targeting a material from animals or humans
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61P—SPECIFIC THERAPEUTIC ACTIVITY OF CHEMICAL COMPOUNDS OR MEDICINAL PREPARATIONS
- A61P35/00—Antineoplastic agents
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K39/00—Medicinal preparations containing antigens or antibodies
- A61K2039/505—Medicinal preparations containing antigens or antibodies comprising antibodies
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K2317/00—Immunoglobulins specific features
- C07K2317/30—Immunoglobulins specific features characterized by aspects of specificity or valency
- C07K2317/31—Immunoglobulins specific features characterized by aspects of specificity or valency multispecific
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K2317/00—Immunoglobulins specific features
- C07K2317/50—Immunoglobulins specific features characterized by immunoglobulin fragments
- C07K2317/56—Immunoglobulins specific features characterized by immunoglobulin fragments variable (Fv) region, i.e. VH and/or VL
- C07K2317/565—Complementarity determining region [CDR]
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K2317/00—Immunoglobulins specific features
- C07K2317/70—Immunoglobulins specific features characterized by effect upon binding to a cell or to an antigen
- C07K2317/77—Internalization into the cell
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K2317/00—Immunoglobulins specific features
- C07K2317/90—Immunoglobulins specific features characterized by (pharmaco)kinetic aspects or by stability of the immunoglobulin
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K2317/00—Immunoglobulins specific features
- C07K2317/90—Immunoglobulins specific features characterized by (pharmaco)kinetic aspects or by stability of the immunoglobulin
- C07K2317/92—Affinity (KD), association rate (Ka), dissociation rate (Kd) or EC50 value
Abstract
Description
本出願は、2019年6月7日に出願された米国特許出願第62/858,932号および2019年8月16日に出願された米国特許出願第62/888,384号の優先権を主張する。これらの出願の各内容は、参照によりそれらの全体が本明細書に組み込まれる。
(iii)配列番号401の重鎖可変ドメイン、ならびに配列番号450または451のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、ならびに/あるいは(f)配列番号471、配列番号515、配列番号518、配列番号519、配列番号520、配列番号521、配列番号522、配列番号524、配列番号526、配列番号528、配列番号531、配列番号533、配列番号535、もしくは配列番号536の軽鎖可変ドメイン、および/または配列番号470、配列番号473、配列番号476、配列番号478、配列番号481、配列番号483、配列番号484、配列番号485、配列番号486、配列番号488、配列番号489、配列番号491、配列番号493、配列番号494、配列番号495、配列番号498、配列番号503、配列番号506、配列番号508、配列番号510、配列番号511、もしくは配列番号512の重鎖可変ドメインであって、第1の抗原結合ドメインは(i)配列番号471の軽鎖可変ドメイン、および配列番号470の重鎖可変ドメイン、(ii)配列番号471の軽鎖可変ドメイン、ならびに配列番号473、476、478、481、483~486、488、489、491、493~495、498、503、506、508、および510~512のうちの1つではない重鎖可変ドメイン、または(iii)配列番号470の重鎖可変ドメイン、ならびに配列番号515、518~522、524、526、528、531、533、535、および536のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、ならびに(g)配列番号538、配列番号581、配列番号587、配列番号591、配列番号599、配列番号600、もしくは配列番号604の軽鎖可変ドメイン、および/または配列番号537、配列番号539、配列番号542、配列番号544、配列番号545、配列番号552、配列番号553、配列番号556、配列番号557、配列番号558、配列番号564、配列番号566、配列番号567、配列番号572、配列番号573、もしくは配列番号575の重鎖可変ドメインであって、第1の抗原結合ドメインは、(i)配列番号538の軽鎖可変ドメイン、および配列番号537の重鎖可変ドメイン、(ii)配列番号538の軽鎖可変ドメイン、ならびに配列番号539、542、544、545、552、553、556~558、564、566、567、572、573、および575のうちの1つではない重鎖可変ドメイン、または(iii)配列番号537の重鎖可変ドメイン、ならびに配列番号581、587、591、599、600、および604のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン。
,000~約45,000、約5,000~約40,000、約5,000~約35,000、約5,000~約30,000、約5,000~約25,000、約5,000~約20,000、約5,000~約15,000、約5,000~約10,000、約5,000~約7,500、約7,500~約10,000,000、約7,500~約9,000,000、約7,500~約8,000,000、約7,500~約7,000,000、約7,500~約6,000,000、約7,500~約5,000,000、約7,500~約4,000,000、約7,500~約3,000,000、約7,500~約2,000,000、約7,500~約1,000,000、約7,500~約800,000、約7,500~約600,000、約7,500~約400,000、約7,500~約200,000、約7,500~約100,000、約7,500~約80,000、約7,500~約75,000、約7,500~約70,000、約7,500~約65,000、約7,500~約60,000、約7,500~約55,000、約7,500~約50,000、約7,500~約45,000、約7,500~約40,000、約7,500~約35,000、約7,500~約30,000、約7,500~約25,000、約7,500~約20,000、約7,500~約15,000、約7,500~約10,000、約10,000~約10,000,000、約10,000~約9,000,000、約10,000~約8,000,000、約10,000~約7,000,000、約10,000~約6,000,000、約10,000~約5,000,000、約10,000~約4,000,000、約10,000~約3,000,000、約10,000~約2,000,000、約10,000~約1,000,000、約10,000~約800,000、約10,000~約600,000、約10,000~約400,000、約10,000~約200,000、約10,000~約100,000、約10,000~約80,000、約10,000~約75,000、約10,000~約70,000、約10,000~約65,000、約10,000~約60,000、約10,000~約55,000、約10,000~約50,000、約10,000~約45,000、約10,000~約40,000、約10,000~約35,000、約10,000~約30,000、約10,000~約25,000、約10,000~約20,000、約10,000~約15,000、約15,000~約10,000,000、約15,000~約9,000,000、約15,000~約8,000,000、約15,000~約7,000,000、約15,000~約6,000,000、約15,000~約5,000,000、約15,000~約4,000,000、約15,000~約3,000,000、約15,000~約2,000,000、約15,000~約1,000,000、約15,000~約800,000、約15,000~約600,000、約15,000~約400,000、約15,000~約200,000、約15,000~約100,000、約15,000~約80,000、約15,000~約75,000、約15,000~約70,000、約15,000~約65,000、約15,000~約60,000、約15,000~約55,000、約15,000~約50,000、約15,000~約45,000、約15,000~約40,000、約15,000~約35,000、約15,000~約30,000、約15,000~約25,000、約15,000~約20,000、約20,000~約10,000,000、約20,000~約9,000,000、約20,000~約8,000,000、約20,000~約7,000,000、約20,000~約6,000,000、約20,000~約5,000,000、約20,000~約4,000,000、約20,000~約3,000,000、約20,000~約2,000,000、約20,000~約1,000,000、約20,000~約800,000、約20,000~約600,000、約20,000~約400,000、約20,000~約200,000、約20,000~約100,000、約20,000~約80,000、約20,000~約75,000、約20,000~約70,000、約20,000~約65,000、約210,000~約60,000、約20,000~約55,000、約20,000~約50,000、約20,000~約45,000、約20,000~約40,000、約20,000~約35,000、約20,000~約30,000、約20,000~約25,000、約25,000~約10,000,000、約25,000~約9,000,000、約25,000~約8,000,000、約25,000~約7,000,000、約25,000~約6,000,000、約25,000~約5,000,000、約25,000~約4,000,000、約25,000~約3,000,000、約25,000~約2,000,000、約25,000~約1,000,000、約25,000~約800,000、約25,000~約600,000、約25,000~約400,000、約25,000~約200,000、約25,000~約100,000、約25,000~約80,000、約25,000~約75,000、約25,000~約70,000、約25,000~約65,000、約25,000~約60,000、約25,000~約55,000、約25,000~約50,000、約25,000~約45,000、約25,000~約40,000、約25,000~約35,000、約25,000~約30,000、約30,000~約10,000,000、約30,000~約9,000,000、約30,000~約8,000,000、約30,000~約7,000,000、約30,000~約6,000,000、約30,000~約5,000,000、約30,000~約4,000,000、約30,000~約3,000,000、約30,000~約2,000,000、約30,000~約1,000,000、約30,000~約800,000、約30,000~約600,000、約30,000~約400,000、約30,000~約200,000、約30,000~約100,000、約30,000~約80,000、約30,000~約75,000、約30,000~約70,000、約30,000~約65,000、約30,000~約60,000、約30,000~約55,000、約30,000~約50,000、約30,000~約45,000、約30,000~約40,000、約30,000~約35,000、約35,000~約10,000,000、約35,000~約9,000,000、約35,000~約8,000,000、約35,000~約7,000,000、約35,000~約6,000,000、約35,000~約5,000,000、約35,000~約4,000,000、約35,000~約3,000,000、約35,000~約2,000,000、約35,000~約1,000,000、約35,000~約800,000、約35,000~約600,000、約35,000~約400,000、約35,000~約200,000、約35,000~約100,000、約35,000~約80,000、約35,000~約75,000、約35,000~約70,000、約35,000~約65,000、約35,000~約60,000、約35,000~約55,000、約35,000~約50,000、約35,000~約45,000、約35,000~約40,000、約40,000~約10,000,000、約40,000~約9,000,000、約40,000~約8,000,000、約40,000~約7,000,000、約40,000~約6,000,000、約40,000~約5,000,000、約40,000~約4,000,000、約40,000~約3,000,000、約40,000~約2,000,000、約40,000~約1,000,000、約40,000~約800,000、約40,000~約600,000、約40,000~約400,000、約40,000~約200,000、約40,000~約100,000、約40,000~約80,000、約40,000~約75,000、約40,000~約70,000、約40,000~約65,000、約40,000~約60,000、約40,000~約55,000、約40,000~約50,000、約40,000~約45,000、約45,000~約10,000,000、約45,000~約9,000,000、約45,000~約8,000,000、約45,000~約7,000,000、約45,000~約6,000,000、約45,000~約5,000,000、約45,000~約4,000,000、約45,000~約3,000,000、約45,000~約2,000,000、約45,000~約1,000,000、約45,000~約800,000、約45,000~約600,000、約45,000~約400,000、約45,000~約200,000、約45,000~約100,000、約45,000~約80,000、約45,000~約75,000、約45,000~約70,000、約45,000~約65,000、約45,000~約60,000、約45,000~約55,000、約45,000~約50,000、約50,000~約10,000,000、約50,000~約9,000,000、約50,000~約8,000,000、約50,000~約7,000,000、約50,000~約6,000,000、約50,000~約5,000,000、約50,000~約4,000,000、約50,000~約3,000,000、約50,000~約2,000,000、約50,000~約1,000,000、約50,000~約800,000、約50,000~約600,000、約50,000~約400,000、約50,000~約200,000、約50,000~約100,000、約50,000~約80,000、約50,000~約75,000、約50,000~約70,000、約50,000~約65,000、約50,000~約60,000、約50,000~約55,000、約55,000~約10,000,000、約55,000~約9,000,000、約55,000~約8,000,000、約55,000~約7,000,000、約55,000~約6,000,000、約55,000~約5,000,000、約55,000~約4,000,000、約55,000~約3,000,000、約55,000~約2,000,000、約55,000~約1,000,000、約55,000~約800,000、約55,000~約600,000、約55,000~約400,000、約55,000~約200,000、約55,000~約100,000、約55,000~約80,000、約55,000~約75,000、約55,000~約70,000、約55,000~約65,000、約55,000~約60,000、約60,000~約10,000,000、約60,000~約9,000,000、約60,000~約8,000,000、約60,000~約7,000,000、約60,000~約6,000,000、約60,000~約5,000,000、約60,000~約4,000,000、約60,000~約3,000,000、約60,000~約2,000,000、約60,000~約1,000,000、約60,000~約800,000、約60,000~約600,0
00、約60,000~約400,000、約60,000~約200,000、約60,000~約100,000、約60,000~約80,000、約60,000~約75,000、約60,000~約70,000、約60,000~約65,000、約65,000~約10,000,000、約65,000~約9,000,000、約65,000~約8,000,000、約65,000~約7,000,000、約65,000~約6,000,000、約65,000~約5,000,000、約65,000~約4,000,000、約65,000~約3,000,000、約65,000~約2,000,000、約65,000~約1,000,000、約65,000~約800,000、約65,000~約600,000、約65,000~約400,000、約65,000~約200,000、約65,000~約100,000、約65,000~約80,000、約65,000~約75,000、約65,000~約70,000、約70,000~約10,000,000、約70,000~約9,000,000、約70,000~約8,000,000、約70,000~約7,000,000、約70,000~約6,000,000、約70,000~約5,000,000、約70,000~約4,000,000、約70,000~約3,000,000、約70,000~約2,000,000、約70,000~約1,000,000、約70,000~約800,000、約70,000~約600,000、約70,000~約400,000、約70,000~約200,000、約70,000~約100,000、約70,000~約90,000、約70,000~約80,000、約80,000~約10,000,000、約80,000~約9,000,000、約80,000~約8,000,000、約80,000~約7,000,000、約80,000~約6,000,000、約80,000~約5,000,000、約80,000~約4,000,000、約80,000~約3,000,000、約80,000~約2,000,000、約80,000~約1,000,000、約80,000~約800,000、約80,000~約600,000、約80,000~約400,000、約80,000~約200,000、約80,000~約100,000、約80,000~約90,000、約90,000~約10,000,000、約90,000~約9,000,000、約90,000~約8,000,000、約90,000~約7,000,000、約90,000~約6,000,000、約90,000~約5,000,000、約90,000~約4,000,000、約90,000~約3,000,000、約90,000~約2,000,000、約90,000~約1,000,000、約90,000~約800,000、約90,000~約600,000、約90,000~約400,000、約90,000~約200,000、約90,000~約100,000、約100,000~約10,000,000、約100,000~約9,000,000、約100,000~約8,000,000、約100,000~約7,000,000、約100,000~約6,000,000、約100,000~約5,000,000、約100,000~約4,000,000、約100,000~約3,000,000、約100,000~約2,000,000、約100,000~約1,000,000、約100,000~約800,000、約100,000~約600,000、約100,000~約400,000、約100,000~約200,000、約200,000~約10,000,000、約200,000~約9,000,000、約200,000~約8,000,000、約200,000~約7,000,000、約200,000~約6,000,000、約200,000~約5,000,000、約200,000~約4,000,000、約200,000~約3,000,000、約200,000~約2,000,000、約200,000~約1,000,000、約200,000~約800,000、約200,000~約600,000、約200,000~約400,000、約400,000~約10,000,000、約400,000~約9,000,000、約400,000~約8,000,000、約400,000~約7,000,000、約400,000~約6,000,000、約400,000~約5,000,000、約400,000~約4,000,000、約400,000~約3,000,000、約400,000~約2,000,000、約400,000~約1,000,000、約400,000~約800,000、約400,000~約600,000、約600,000~約10,000,000、約600,000~約9,000,000、約600,000~約8,000,000、約600,000~約7,000,000、約600,000~約6,000,000、約600,000~約5,000,000、約600,000~約4,000,000、約600,000~約3,000,000、約600,000~約2,000,000、約600,000~約1,000,000、約600,000~約800,000、約800,000~約10,000,000、約800,000~約9,000,000、約800,000~約8,000,000、約800,000~約7,000,000、約800,000~約6,000,000、約800,000~約5,000,000、約800,000~約4,000,000、約800,000~約3,000,000、約800,000~約2,000,000、約800,000~約1,000,000、約1,000,000~約10,000,000、約1,000,000~約9,000,000、約1,000,000~約8,000,000、約1,000,000~約7,000,000、約1,000,000~約6,000,000、約1,000,000~約5,000,000、約1,000,000~約4,000,000、約1,000,000~約3,000,000、約1,000,000~約2,000,000、約2,000,000~約10,000,000、約2,000,000~約9,000,000、約2,000,000~約8,000,000、約2,000,000~約7,000,000、約2,000,000~約6,000,000、約2,000,000~約5,000,000、約2,000,000~約4,000,000、約2,000,000~約3,000,000、約3,000,000~約10,000,000、約3,000,000~約9,000,000、約3,000,000~約8,000,000、約3,000,000~約7,000,000、約3,000,000~約6,000,000、約3,000,000~約5,000,000、約3,000,000~約4,000,000、約4,000,000~約10,000,000、約4,000,000~約9,000,000、約4,000,000~約8,000,000、約4,000,000~約7,000,000、約4,000,000~約6,000,000、約4,000,000~約5,000,000、約5,000,000~約10,000,000、約5,000,000~約9,000,000、約5,000,000~約8,000,000、約5,000,000~約7,000,000、約5,000,000~約6,000,000、約6,000,000~約10,000,000、約6,000,000~約9,000,000、約6,000,000~約8,000,000、約6,000,000~約7,000,000、約7,000,000~約10,000,000、約7,000,000~約9,000,000、約7,000,000~約8,000,000、約8,000,000~約10,000,000、約8,000,000~約9,000,000、または約9,000,000~約10,000,000のDLL3が存在することができる。
本明細書に記載のABPCのうちのいずれかのいくつかの例では、第1の抗原結合ドメインは、配列番号83を含む重鎖可変ドメインと、配列番号2、配列番号54、配列番号55、配列番号56、配列番号57、配列番号58、配列番号59、配列番号60、配列番号61、配列番号62、配列番号63、配列番号64、配列番号65、配列番号66、配列番号67、配列番号68、配列番号69、配列番号70、配列番号71、配列番号72、配列番号73、配列番号74、配列番号75、配列番号76、配列番号77、配列番号78、配列番号79、または配列番号80を含む軽鎖可変ドメインとを含む。
配列番号237と少なくとも90%(例えば、少なくとも92%、少なくとも94%、少なくとも96%、少なくとも98%、少なくとも99%、または100%)同一である軽鎖可変ドメインであって、25、29、32、33、49、50、90、91、93、および95からなる群から選択される配列番号237の1つ以上(例えば、1、2、3、4、5、6、7、8、9、10、11、12、13、14、15、16、17、18、19、または20)のアミノ酸位置にヒスチジンを含む軽鎖可変ドメインとを含む。
配列番号237と少なくとも90%(例えば、少なくとも92%、少なくとも94%、少なくとも96%、少なくとも98%、少なくとも99%、または100%)同一である軽鎖可変ドメインであって、25、29、32、33、49、50、90、91、93、および95からなる群から選択される配列番号237の1つ以上(例えば、1、2、3、4、5、6、7、8、9、10、11、12、13、14、15、16、17、18、19、または20個)のアミノ酸位置にヒスチジンを含む軽鎖可変ドメインとを含む。
配列番号336と少なくとも90%(例えば、少なくとも92%、少なくとも94%、少なくとも96%、少なくとも98%、少なくとも99%、または100%)同一である軽鎖可変ドメインであって、27、29、32、34、52、53、89、90、91、92、93、94、および96からなる群から選択される配列番号336の1つ以上(例えば、1、2、3、4、5、6、7、8、9、10、11、12、13、14、15、16、17、18、19、または20個)のアミノ酸位置にヒスチジンを含む軽鎖可変ドメインとを含む。
9,000%の増加、約30%~約8,000%の増加、約30%~約7,000%の増加、約30%の増加~約6,000%の増加、約30%の増加~約5,000%の増加、約30%の増加~約4,000%の増加、約30%の増加~約3,000%の増加、約30%の増加約2,000%の増加、約30%の増加~約1,000%の増加、約30%の増加~約500%の増加、約30%の増加~約450%の増加、約30%の増加~約500%の増加400%の増加、約30%の増加~約350%の増加、約30%の増加~約300%の増加、約30%の増加~約250%の増加、約30%の増加~約200%の増加、約30%の増加~約180%の増加、約30%の増加~約160%の増加、約30%の増加~約140%の増加、約30%の増加~約120%の増加、約30%の増加~約100%の増加、約30%の増加~約95%の増加、約30%の増加~約90%の増加、約30%の増加~約85%の増加、約30%~約80%の増加、約30%~約75%の増加、約30%~約70%の増加、約30%~約65%の増加、約30%の増加~約60%の増加、約30%の増加~約55%の増加、約30%の増加~約50%の増加、約30%の増加~約45%の増加、約30%約40%の増加、約30%の増加~約35%の増加、約35%~約10,000%の増加、約35%~約9,000%の増加、約35%~約8,000%の増加、約35%~約7,000%の増加、約35%の増加~約6,000%の増加、約35%の増加~約5,000%の増加、約35%の増加~約4,000%の増加、約35%の増加~約3,000%の増加、約35%の増加約2,000%の増加、約35%の増加~約1,000%の増加、約35%の増加~約500%の増加、約35%の増加~約450%の増加、約35%の増加~約500%の増加400%の増加、約35%の増加~約350%の増加、約35%の増加~約300%の増加、約35%の増加~約250%の増加、約35%の増加~約200%の増加、約35%の増加~約180%の増加、約35%の増加~約160%の増加、約35%の増加~約140%の増加、約35%の増加~約120%の増加、約35%の増加~約100%の増加、約35%の増加~約95%の増加、約35%の増加~約90%の増加、約35%の増加~約85%の増加、約35%~約80%の増加、約35%~約75%の増加、約35%~約70%の増加、約35%~約65%の増加、約35%の増加~約60%の増加、約35%の増加~約55%の増加、約35%の増加~約50%の増加、約35%の増加~約45%の増加、約35%約40%の増加に増加し、約40%~約10,000%の増加、約40%~約9,000%の増加、約40%~約8,000%の増加、約40%~約7,000%の増加、約40%の増加~約6,000%の増加、約40%の増加~約5,000%の増加、約40%の増加~約4,000%の増加、約40%の増加~約3,000%の増加、約40%の増加約2,000%の増加、約40%の増加~約1,000%の増加、約40%の増加~約500%の増加、約40%の増加~約450%の増加、約40%の増加~約400%の増加、約40%の増加~約350%の増加、約40%の増加~約300%の増加、約40%の増加~約250%の増加、約40%の増加~約200%の増加%の増加、約40%の増加~約180%の増加、約40%の増加~約160%の増加、約40%の増加~約140%の増加、約40%の増加~約120%の増加、約40%の増加~約100%の増加、約40%の増加~約95%の増加、約40%の増加~約90%の増加、約40%の増加~約85%の増加、約40%~約80%の増加、約40%~約75%の増加、約40%~約70%の増加、約40%~約65%の増加、約40%の増加~約60%の増加、約40%の増加~約55%の増加、約40%の増加~約50%の増加、約40%の増加~約45%の増加、約45%~約10,000%の増加、約45%~約9,000%の増加、約45%~約8,000%の増加、約45%~約7,000%の増加、約45%の増加~約6,000%の増加、約45%の増加~約5,000%の増加、約45%の増加~約4,000%の増加、約45%の増加~約3,000%の増加、約45%の増加約2,000%の増加、約45%の増加~約1,000%の増加、約45%の増加~約500%の増加、約45%の増加~約450%の増加、約45%の増加~約400%の増加、約45%の増加~約350%の増加、約45%の増加~約300%の増加、約45%の増加~約250%の増加、約45%の増加~約200%の増加%の増加、約45%の増加~約180%の増加、約45%の増加~約160%の増加、約45%の増加~約140%の増加、約45%の増加~約120%の増加、約45%の増加~約100%の増加、約45%の増加~約95%の増加、約45%の増加~約90%の増加、約45%の増加~約85%の増加、約45%~約80%の増加、約45%~約75%の増加、約45%~約70%の増加、約45%~約65%の増加、約45%の増加~約60%の増加、約45%の増加~約55%の増加、約45%の増加~約50%の増加、約50%~約10,000%の増加、約50%~約9,000%の増加、約50%~約8,000%の増加、約50%~約7,000%の増加、約50%の増加~約6,000%の増加、約50%の増加~約5,000%の増加、約50%の増加~約4,000%の増加、約50%の増加~約3,000%の増加、約50%の増加約2,000%の増加、約50%の増加~約1,000%の増加、約50%の増加~約500%の増加、約50%の増加~約450%の増加、約50%の増加~約500%の増加400%の増加、約50%の増加~約350%の増加、約50%の増加~約300%の増加、約50%の増加~約250%の増加、約50%の増加~約200%の増加%の増加、約50%の増加~約180%の増加、約50%の増加~約160%の増加、約50%の増加~約140%の増加、約50%の増加~約120%の増加、約50%の増加~約100%の増加、約50%の増加~約95%の増加、約50%の増加~約90%の増加、約50%の増加~約85%の増加、約50%~約80%の増加、約50%~約75%の増加、約50%~約70%の増加、約50%~約65%の増加、約50%の増加~約60%の増加、約50%の増加~約55%の増加、約55%~約10,000%の増加、約55%~約9,000%の増加、約55%~約8,000%の増加、約55%~約7,000%の増加、約55%の増加~約6,000%の増加、約55%の増加~約5,000%の増加、約55%の増加~約4,000%の増加、約55%の増加~約3,000%の増加、約55%の増加約2,000%の増加、約55%の増加~約1,000%の増加、約55%の増加~約500%の増加、約55%の増加~約450%の増加、約55%の増加~約400%の増加、約55%の増加~約350%の増加、約55%の増加~約300%の増加、約55%の増加~約250%の増加、約55%の増加~約200%の増加、約55%の増加~約180%の増加、約55%の増加~約160%の増加、約55%の増加~約140%の増加、約55%の増加~約120%の増加、約55%の増加~約100%の増加、約55%の増加~約95%の増加、約55%の増加~約90%の増加、約55%の増加~約85%の増加、約55%~約80%の増加、約55%~約75%の増加、約55%~約70%の増加、約55%~約65%の増加、約55%の増加~約60%の増加し、約60%~約10,000%の増加、約60%~約9,000%の増加、約60%~約8,000%の増加、約60%~約7,000%の増加、約60%の増加~約6,000%の増加、約60%の増加~約5,000%の増加、約60%の増加~約4,000%の増加、約60%の増加~約3,000%の増加、約60%の増加約2,000%の増加、約60%の増加~約1,000%の増加、約60%の増加~約500%の増加、約60%の増加~約450%の増加、約60%の増加~約400%の増加、約60%の増加~約350%の増加、約60%の増加~約300%の増加、約60%の増加~約250%の増加、約60%の増加~約200%の増加%の増加、約60%の増加~約180%の増加、約60%の増加~約160%の増加、約60%の増加~約140%の増加、約60%の増加~約120%の増加簡単、約60%~約100%の増加、約60%~約95%の増加、約60%~約90%の増加、約60%~約85%の増加、約60%~約80%の増加、約60%~約75%の増加、約60%~約70%の増加、約60%~約65%の増加、約65%~約10,000%の増加、約65%~約9,000%の増加、約65%~約8,000%の増加、約65%~約7,000%の増加、約65%の増加~約6,000%の増加、約65%の増加~約5,000%の増加、約65%の増加~約4,000%の増加、約65%の増加~約3,000%の増加、約65%の増加約2,000%の増加、約65%の増加~約1,000%の増加、約65%の増加~約500%の増加、約65%の増加~約450%の増加、約65%の増加~約400%の増加、約65%の増加~約350%の増加、約65%の増加~約300%の増加、約65%の増加~約250%の増加、約65%の増加~約200%の増加%の増加、約65%の増加~約180%の増加、約65%の増加~約160%の増加、約65%の増加~約140%の増加、約65%の増加~約120%の増加簡単、約65%~約100%の増加、約65%~約95%の増加、約65%~約90%の増加、約65%~約85%の増加、約65%~約80%の増加、約65%~約75%の増加、約65%~約70%の増加、約70%~約10,000%の増加、約70%~約9,000%の増加、約70%~約8,000%の増加、約70%~約7,000%の増加、約70%の増加~約6,000%の増加、約70%の増加~約5,000%の増加、約70%の増加~約4,000%の増加、約70%の増加~約3,000%の増加、約70%の増加約2,000%の増加、約70%の増加~約1,000%の増加、約70%の増加~約500%の増加、約70%の増加~約450%の増加、約70%の増加~約400%の増加、約70%の増加~約350%の増加、約70%の増加~約300%の増加、約70%の増加~約250%の増加、約70%の増加~約200%の増加%の増加、約70%の増加~約180%の増加、約70%の増加~約160%の増加、約70%の増加~約140%の増加、約70%の増加~約120%の増加、約70%の増加~約100%の増加、約70%の増加~約95%の増加、約70%の増加~約90%の増加、約70%の増加~約85%の増加、約70%~約80%の増加、約70%~約75%の増加、約75%~約10,000%の増加、約75%~約9,000%の増加、約75%~約8,000%の増加、約75%~約7,000%の増加、約75%の増加~約6,000%の増加、約75%の増加~約5,000%の増加、約75%の増加~約4,000%の増加、約75%の増加~約3,000%の増加、約75%の増加約2,000%の増加、約75%の増加~約1,000%の増加、約75%の増加~約500%の増加、約75%の増加~約450%の増加、約75%の増加~約400%の増加、約75%の増加~約350%の増加、約75%の増加~約300%の増加、約75%の増加~約250%の増加、約75%の増加~約200%の増加、約75%の増加~約180%の増加、約75%の増加~約160%の増加、約75%の増加~約140%の増加、約75%の増加~約120%の増加簡単、約75%~約100%の増加、約75%~約95%の増加、約75%~約90%の増加、約75%~約85%の増加、約75%~約80%の増加、約80%~約10,000%の増加、約80%~約9,000%の増加、約80%~約8,000%の増加、約80%~
約7,000%の増加、約80%の増加~約6,000%の増加、約80%の増加~約5,000%の増加、約80%の増加~約4,000%の増加、約80%の増加~約3,000%の増加、約80%の増加約2,000%の増加、約80%の増加~約1,000%の増加、増加、約80%の増加~約500%の増加、約80%の増加~約450%の増加、約80%の増加約400%の増加、約80%の増加~約350%の増加、約80%の増加~約300%の増加、約80%の増加~約250%の増加、約80%の増加~約300%の増加200%の増加、約80%の増加~約180%の増加、約80%の増加~約160%の増加、約80%の増加~約140%の増加、約80%の増加~約120%の増加、約80%の増加~約100%の増加、約80%の増加~約95%の増加、約80%の増加~約90%の増加、約80%の増加~約85%の増加、約85%~約10,000%の増加、約85%~約9,000%の増加、約85%~約8,000%の増加、約85%~約7,000%の増加、約85%の増加~約6,000%の増加、約85%の増加~約5,000%の増加、約85%の増加~約4,000%の増加、約85%の増加~約3,000%の増加、約85%の増加約2,000%の増加、約85%の増加~約1,000%の増加、約85%の増加~約500%の増加、約85%の増加~約450%の増加、約85%の増加~約500%の増加400%の増加、約85%の増加~約350%の増加、約85%の増加~約300%の増加、約85%の増加~約250%の増加、約85%の増加~約200%の増加%の増加、約85%の増加~約180%の増加、約85%の増加~約160%の増加、約85%の増加~約140%の増加、約85%の増加~約120%の増加簡単に、約85%~約100%の増加、約85%~約95%の増加、約85%~約90%の増加、約90%~約10,000%の増加、約90%の増加~約9,000%の増加、約90%の増加~約8,000%の増加、約90%の増加~約7,000%の増加、約90%の増加~約6,000%の増加、約90%の増加~約5,000%の増加、約90%の増加~約4,000%の増加、約90%の増加~約3,000%の増加、約90%の増加~約2,000%の増加、約90%の増加約1,000%の増加、約90%の増加~約500%の増加、約90%の増加~約450%の増加、約90%の増加~約400%の増加、約90%の増加~約350%の増加、約90%の増加~約300%の増加、約90%の増加~約250%の増加、約90%の増加~約200%の増加、約90%の増加~約180%の増加、約90%の増加~約160%の増加、約90%の増加~約140%の増加、約90%の増加~約120%の増加、約90%の増加~約100%の増加、約90%の増加~約95%の増加、約95%~約10,000%の増加、約95%~約9,000%の増加、約95%~約8,000%の増加、約95%~約7,000%の増加、約95%の増加~約6,000%の増加、約95%の増加~約5,000%の増加、約95%の増加~約4,000%の増加、約95%の増加~約3,000%の増加、約95%の増加約2,000%の増加、約95%の増加~約1,000%の増加、約95%の増加~約500%の増加、約95%の増加~約450%の増加、約95%の増加~約400%の増加、約95%の増加~約350%の増加、約95%の増加~約300%の増加、約95%の増加~約250%の増加、約95%の増加~約200%の増加%の増加、約95%の増加~約180%の増加、約95%の増加~約160%の増加、約95%の増加~約140%の増加、約95%の増加~約120%の増加簡単に、約95%~約100%の増加、約100%~約10,000%の増加、約100%~約9,000%の増加、約100%~約8,000%の増加、約100%の増加~約7,000%の増加、約100%の増加~約6,000%の増加、約100%の増加~約5,000%の増加、約100%の増加~約4,000%の増加、約100%の増加~約3,000%の増加、約100%の増加~約2,000%の増加、約100%の増加~約1,000%の増加、約100%の増加~約500%の増加、約100%の増加約450%の増加、約100%の増加~約400%の増加、約100%の増加~約350%の増加、約100%の増加~約300%の増加、約100%の増加~約250%の増加、約100%の増加~約200%の増加、約100%の増加~約180%の増加、約100%の増加~約160%の増加、約100%の増分約140%の増加、約100%の増加~約120%の増加、約120%~約10,000%の増加、約120%~約9,000%の増加、約120%~約8,000%の増加、約120%~約7,000%の増加、約120%の増加~約6,000%の増加、約120%の増加~約5,000%の増加、約120%の増加~約4,000%の増加、約120%の増加~約3,000%の増加、約120%の増加約2,000%の増加、約120%の増加~約1,000%の増加、約120%の増加~約500%の増加、約120%の増加~約450%の増加、約120%の増加~約400%の増加、約120%の増加~約350%の増加、約120%の増加~約300%の増加、約120%の増加~約250%の増加、約120%の増加~約200%の増加%の増加、約120%の増加~約180%の増加、約120%の増加~約160%の増加、約120%の増加~約140%の増加、約140%の増加約10,000%の増加、約140%の増加~約9,000%の増加、約140%の増加~約8,000%の増加、約140%の増加~約7,000%の増加、約140%の増加~約6,000%の増加、約140%の増加~約5,000%の増加、約140%の増加~約4,000%の増加、約140%の増加~約3,000%の増加、約140%の増加~約2,000%の増加、約140%の増加~約1,000%の増加、約140%の増加~約500%の増加、約140%の増加~約450%の増加、約140%の増加~約400%の増加、約140%の増加~約350%の増加、約140%の増加~約300%の増加、約140%の増加~約250%の増加、約140%の増加~約200%の増加、約140%の増加~約180%の増加、約140%の増加~約160%の増加、約160%の増加~約10,000%の増加、約160%の増加~約9,000%の増加、約160%の増加~約8,000%の増加、約160%の増加~約7,000%の増加、約160%の増加~約6,000%の増加、約160%の増加~約5,000%の増加、約160%~約4,000%の増加、約160%~約3,000%の増加、約160%~約2,000%の増加、約160%~約1,000%の増加、約160%の増加~約500%の増加、約160%の増加~約450%の増加、約160%の増加~約400%の増加、約160%の増加~約350%の増加、約160%約300%の増加、約160%の増加~約250%の増加、約160%の増加~約200%の増加、約160%の増加~約180%の増加、約180%の増加約10,000%の増加、約180%の増加~約9,000%の増加、約180%の増加~約8,000%の増加、約180%の増加~約7,000%の増加、約180%の増加~約6,000%の増加、約180%の増加~約5,000%の増加、約180%の増加~約4,000%の増加、約180%の増加~約3,000%の増加、約180%約2,000%の増加、約180%の増加~約1,000%の増加、約180%の増加~約500%の増加、約180%の増加~約450%の増加、約180%の増加~約400%の増加、約180%の増加~約350%の増加、約180%の増加~約300%の増加、約180%の増加~約250%の増加、約180%の増加~約200%の増加、約200%の増加~約10,000%の増加、約200%の増加~約9,000%の増加、約200%の増加~約8,000%の増加、約200%の増加~約7,000%の増加、約200%~約6,000%の増加、約200%~約5,000%の増加、約200%~約4,000%の増加、約200%の増加~約3,000%の増加、約200%の増加~約2,000%の増加、約200%の増加~約1,000%の増加、約200%の増加~約500%の増加、約200%の増加~約200%の増加450%の増加、約200%の増加~約400%の増加、約200%の増加~約350%の増加、約200%の増加~約300%の増加、約200%の増加~約250%の増加、約250%~約10,000%の増加、約250%~約9,000%の増加、約250%~約8,000%の増加、約250%~約7,000%の増加、約250%の増加~約6,000%の増加、約250%の増加~約5,000%の増加、約250%の増加~約4,000%の増加、約250%の増加~約3,000%の増加、約250%の増加約2,000%の増加、約250%の増加~約1,000%の増加、約250%の増加~約500%の増加、約250%の増加~約450%の増加、約250%の増加~約250%の増加400%の増加、約250%の増加~約350%の増加、約250%の増加~約300%の増加、約300%の増加~約10,000%の増加、約300%の増加~約9,000%の増加、約300%の増加~約8,000%の増加、約300%の増加~約7,000%の増加、約300%の増加~約6,000%の増加、約300%約5,000%の増加、約300%の増加~約4,000%の増加、約300%の増加~約3,000%の増加、約300%の増加~約2,000%の増加、約300%の増加~約1,000%の増加、約300%の増加~約500%の増加、約300%の増加~約450%の増加、約300%の増加~約400%の増加、約300%の増加~約350%の増加、約350%の増加~約10,000%の増加、約350%の増加~約9,000%の増加、約350%の増加~約8,000%の増加、約350%の増加~約7,000%の増加、約350%の増加~約6,000%の増加、約350%の増加~約5,000%の増加、約350%の増加~約4,000%の増加、約350%の増加~約3,000%の増加、約350%の増加~約2,000%の増加、約350%の増加~約1,000%の増加、約350%の増加~約500%の増加、約350%の増加~約450%の増加、約350%の増加~約400%の増加、約400%の増加~約10,000%の増加、約400%の増加~約9,000%の増加、約400%の増加~約8,000%の増加、約400%の増加~約7,000%の増加、約400%の増加~約6,000%の増加、約400%の増加~約5,000%の増加、約400%の増加~約4,000%の増加、約400%の増加~約3,000%の増加、約400%の増加~約2,000%の増加、約400%の増加~約1,000%の増加、約400%の増加~約500%の増加、約400%~約450%の増加、約450%~約10,000%の増加、約450%~約9,000%の増加、約450%~約8,000%の増加、約450%の増加~約7,000%の増加、約450%の増加~約6,000%の増加、約450%の増加~約5,000%の増加、約450%の増加~約4,000%の増加、約450%の増加~約3,000%の増加、約450%の増加~約2,000%の増加、約450%の増加~約1,000%の増加、約450%の増加~約500%の増加、約500%~約10,000%の増加、約500%~約9,000%の増加、約500%~約8,000%の増加、約500%~約7,000%の増加、約500%の増加~約6,000%の増加、約500%の増加~約5,000%の増加、約500%の増加~約4,000%の増加、約500%の増加~約3,000%の増加、約500%の増加約2,000%の増加、約500%の増加~約1,000%の増加、約1,
000%の増加~約10,000%の増加、約1,000%の増加~約9,000%の増加、約1,000%の増加~約8,000%の増加、約1,000%の増加~約7,000%の増加、約1,000%の増加~約6,000%の増加、約1,000%の増加~約5,000%の増加、約1,000%の増加~約4,000%の増加、約1,000%の増加~約3,000%の増加、約1,000%の増加~約2,000%の増加、約2,000%の増加~約10,000%の増加、約2,000%の増加~約9,000%の増加、約2,000%の増加~約8,000%の増加、約2,000%の増加~約7,000%の増加、約2,000%の増加~約6,000%の増加、約2,000%の増加~約5,000%の増加、約2,000%の増加~約4,000%の増加、約2,000%の増加~約3,000%の増加、約3,000%の増加~約10,000%の増加、約3,000%の増加~約9,000%の増加、約3,000%の増加~約8,000%の増加、約3,000%の増加~約7,000%の増加、約3,000%の増加~約6,000%の増加、約3,000%の増加~約5,000%の増加、約3,000%の増加~約4,000%の増加、約4,000%の増加~約10,000%の増加、約4,000%の増加~約9,000%の増加、約4,000%の増加~約8,000%の増加、約4,000%の増加~約7,000%の増加、約4,000%の増加~約6,000%の増加、約4,000%の増加~約5,000%の増加、約5,000%の増加~約10,000%の増加、約5,000%の増加~約9,000%の増加、約5,000%の増加~約8,000%の増加、約5,000%の増加~約7,000%の増加、約5,000%の増加~約6,000%の増加、約6,000%の増加~約10,000%の増加、約6,000%の増加~約9,000%の増加、約6,000%約8,000%の増加、約6,000%の増加~約7,000%の増加、約7,000%の増加~約10,000%の増加、約7,000%の増加~約9,000%の増加、約7,000%の増加~約7,000%の増加8,000%の増加、約8,000%の増加~約10,000%の増加、約8,000%の増加~約9,000%の増加、または約9,000%~約10,000%の増加)を提供することができる。
1.4倍の増加、約0.6倍の増加~約1.2倍の増加、約0.6倍の増加~約1.0倍の増加、約0.6倍の増加~約0.9倍の増加、約0.6倍の増加~約0.8倍の増加、約0.7倍の増加~約100倍の増加、約0.7倍の増加~約90倍の増加、約0.7倍の増加~約80倍の増加、約0.7倍の増加~約70倍の増加、約0.7倍の増加~約60倍の増加、約0.7倍の増加~約50倍の増加、約0.7倍の増加~約40倍の増加、約0.7倍の増加~約30倍の増加、約0.7倍の増加~約20倍の増加、約0.7倍の増加~約10倍の増加、約0.7倍の増加~約9.5倍の増加、約0.7倍の増加~約9.0倍の増加、約0.7倍の増加~約8.5倍の増加、約0.7倍の増加~約8.0倍の増加、約0.7倍の増加~約7.5倍の増加、約0.7倍の増加~約7.0倍の増加、約0.7倍の増加~約6.5倍の増加、約0.7倍の増加~約6.0倍の増加、約0.7倍の増加~約5.5倍の増加、約0.7倍の増加~約5.0倍の増加、約0.7倍の増加~約4.5倍の増加、約0.7倍の増加~約4.0倍の増加、約0.7倍の増加~約3.5倍の増加、約0.7倍の増加~約3.0倍の増加、約0.7倍の増加~約2.8倍の増加、約0.7倍の増加~約2.6倍の増加、約0.7倍の増加~約2.5倍の増加、約0.7倍の増加~約2.4倍の増加、約0.7倍の増加~約2.2倍の増加、約0.7倍の増加~約2.0倍の増加、約0.7倍の増加~約1.8倍の増加、約0.7倍の増加~約1.6倍の増加、約0.7倍の増加~約1.5倍の増加、約0.7倍の増加~約1.4倍の増加、約0.7倍の増加~約1.2倍の増加、約0.7倍の増加~約1.0倍の増加、約0.7倍の増加~約0.9倍の増加、約0.8倍の増加~約100倍の増加、約0.8倍の増加~約90倍の増加、約0.8倍の増加~約80倍の増加、約0.8倍の増加~約70倍の増加、約0.8倍の増加~約60倍の増加、約0.8倍の増加~約50倍の増加、約0.8倍の増加~約40倍の増加、約0.8倍の増加~約30倍の増加、約0.8倍の増加~約20倍の増加、約0.8倍の増加~約10倍の増加、約0.8倍の増加~約9.5倍の増加、約0.8倍の増加~約9.0倍の増加、約0.8倍の増加~約8.5倍の増加、約0.8倍の増加~約8.0倍の増加、約0.8倍の増加~約7.5倍の増加、約0.8倍の増加~約7.0倍の増加、約0.8倍の増加~約6.5倍の増加、約0.8倍の増加~約6.0倍の増加、約0.8倍の増加~約5.5倍の増加、約0.8倍の増加~約5.0倍の増加、約0.8倍の増加~約4.5倍の増加、約0.8倍の増加~約4.0倍の増加、約0.8倍の増加~約3.5倍の増加、約0.8倍の増加~約3.0倍の増加、約0.8倍の増加~約2.8倍の増加、約0.8倍の増加~約2.6倍の増加、約0.8倍の増加~約2.5倍の増加、約0.8倍の増加~約2.4倍の増加、約0.8倍の増加~約2.2倍への増加、約0.8倍の増加~約2.0倍の増加、約0.8倍の増加~約1.8倍の増加、約0.8倍の増加~約1.6倍の増加、約0.8倍の増加~約1.5倍の増加、約0.8倍の増加~約1.4倍の増加、約0.8倍の増加~約1.2倍の増加、約0.8倍の増加~約1.0倍の増加、約1.0倍の増加~約100倍の増加、約1.0倍の増加~約90倍の増加、約1.0倍の増加~約80倍の増加、約1.0倍の増加~約70倍の増加、約1.0倍の増加~約60倍の増加、約1.0倍の増加~約50倍の増加、約1.0倍の増加~約40倍の増加、約1.0倍の増加~約30倍の増加、約1.0倍の増加~約20倍の増加、約1.0倍の増加~約10倍の増加、約1.0倍の増加~約9.5倍の増加、約1.0倍の増加~約9.0倍の増加、約1.0倍の増加~約8.5倍の増加、約1.0倍の増加~約8.0倍の増加、約1.0倍の増加~約7.5倍の増加、約1.0倍の増加~約7.0倍の増加、約1.0倍の増加~約6.5倍の増加、約1.0倍の増加~約6.0倍の増加、約1.0倍の増加~約5.5倍の増加、約1.0倍の増加~約5.0倍の増加、約1.0倍の増加~約4.5倍の増加、約1.0倍の増加~約4.0倍の増加、約1.0倍の増加~約3.5倍の増加、約1.0倍の増加~約3.0倍の増加、約1.0倍の増加~約2.8倍の増加、約1.0倍の増加~約2.6倍の増加、約1.0倍の増加~約2.5倍の増加、約1.0倍の増加~約2.4倍の増加、約1.0倍の増加~約2.2倍の増加、約1.0倍の増加~約2.0倍の増加、約1.0倍の増加~約1.8倍の増加、約1.0倍の増加~約1.6倍の増加、約1.0倍の増加~約1.5倍の増加、約1.0倍の増加~約1.4倍の増加、約1.0倍の増加~約1.2倍の増加、約1.2倍の増加~約100倍の増加、約1.2倍の増加~約90倍の増加、約1.2倍の増加~約80倍の増加、約1.2倍の増加~約70倍の増加、約1.2倍の増加~約60倍の増加、約1.2倍の増加~約50倍の増加、約1.2倍の増加~約40倍の増加、約1.2倍の増加~約30倍の増加、約1.2倍の増加~約20倍の増加、約1.2倍の増加~約10倍の増加、約1.2倍の増加~約9.5倍の増加、約1.2倍の増加~約9.0倍の増加、約1.2倍の増加~約8.5倍の増加、約1.2倍の増加~約8.0倍の増加、約1.2倍の増加~約7.5倍の増加、約1.2倍の増加~約7.0倍の増加、約1.2倍の増加~約6.5倍の増加、約1.2倍の増加~約6.0倍の増加、約1.2倍の増加~約5.5倍の増加、約1.2倍の増加~約5.0倍の増加、約1.2倍の増加~約4.5倍の増加、約1.2倍の増加~約4.0倍の増加、約1.2倍の増加~約3.5倍の増加、約1.2倍の増加~約3.0倍の増加、約1.2倍の増加~約2.8倍の増加、約1.2倍の増加~約2.6倍の増加、約1.2倍の増加~約2.5倍の増加、約1.2倍の増加~約2.4倍の増加、約1.2倍の増加~約2.2倍の増加、約1.2倍の増加~約2.0倍の増加、約1.2倍の増加~約1.8倍の増加、約1.2倍の増加~約1.6倍の増加、約1.2倍の増加~約1.5倍の増加、約1.2倍の増加~約1.4倍の増加、約1.4倍の増加~約100倍の増加、約1.4倍の増加~約90倍の増加、約1.4倍の増加~約80倍の増加、約1.4倍の増加~約70倍の増加、約1.4倍の増加~約60倍の増加、約1.4倍の増加~約50倍の増加、約1.4倍の増加~約40倍の増加、約1.4倍の増加~約30倍の増加、約1.4倍の増加~約20倍の増加、約1.4倍の増加~約10倍の増加、約1.4倍の増加~約9.5倍の増加、約1.4倍の増加~約9.0倍の増加、約1.4倍の増加~約8.5倍の増加、約1.4倍の増加~約8.0倍の増加、約1.4倍の増加~約7.5倍の増加、約1.4倍の増加~約7.0倍の増加、約1.4倍の増加~約6.5倍の増加、約1.4倍の増加~約6.0倍の増加、約1.4倍の増加~約5.5倍の増加、約1.4倍の増加~約5.0倍の増加、約1.4倍の増加~約4.5倍の増加、約1.4倍の増加~約4.0倍の増加、約1.4倍の増加~約3.5倍の増加、約1.4倍の増加~約3.0倍の増加、約1.4倍の増加~約2.8倍の増加、約1.4倍の増加~約2.6倍の増加、約1.4倍の増加~約2.5倍の増加、約1.4倍の増加~約2.4倍の増加、約1.4倍の増加~約2.2倍の増加、約1.4倍の増加~約2.0倍の増加、約1.4倍の増加~約1.8倍の増加、約1.4倍の増加~約1.6倍の増加、約1.6倍の増加~約10倍の増加、約1.6倍の増加~約100倍の増加、約1.6倍の増加~約90倍の増加、約1.6倍の増加~約80倍の増加、約1.6倍の増加~約70倍の増加、約1.6倍の増加~約60倍の増加、約1.6倍の増加~約50倍の増加、約1.6倍の増加~約40倍の増加、約1.6倍の増加~約30倍の増加、約1.6倍の増加~約20倍の増加、約1.6倍の増加~約9.5倍の増加、約1.6倍の増加~約9.0倍の増加、約1.6倍の増加~約8.5倍の増加、約1.6倍の増加~約8.0倍の増加、約1.6倍の増加~約7.5倍の増加、約1.6倍の増加~約7.0倍の増加、約1.6倍の増加~約6.5倍の増加、約1.6倍の増加~約6.0倍の増加、約1.6倍の増加~約5.5倍の増加、約1.6倍の増加~約5.0倍の増加、約1.6倍の増加~約4.5倍の増加、約1.6倍の増加~約4.0倍の増加、約1.6倍の増加~約3.5倍の増加、約1.6倍の増加~約3.0倍の増加、約1.6倍の増加~約2.8倍の増加、約1.6倍の増加~約2.6倍の増加、約1.6倍の増加~約2.5倍の増加、約1.6倍の増加~約2.4倍の増加、約1.6倍の増加~約2.2倍の増加、約1.6倍の増加~約2.0倍の増加、約1.6倍の増加~約1.8倍の増加、約1.8倍の増加~約100倍の増加、約1.8倍の増加~約90倍の増加、約1.8倍の増加~約80倍の増加、約1.8倍の増加~約70倍の増加、約1.8倍の増加~約60倍の増加、約1.8倍の増加~約50倍の増加、約1.8倍の増加~約40倍の増加、約1.8倍の増加~約30倍の増加、約1.8倍の増加~約20倍の増加、約1.8倍の増加~約10倍の増加、約1.8倍の増加~約9.5倍の増加、約1.8倍の増加~約9.0倍の増加、約1.8倍の増加~約8.5倍の増加、約1.8倍の増加~約8.0倍の増加、約1.8倍の増加~約7.5倍の増加、約1.8倍の増加~約7.0倍の増加、約1.8倍の増加~約6.5倍の増加、約1.8倍の増加~約6.0倍の増加、約1.8倍の増加~約5.5倍の増加、約1.8倍の増加~約5.0倍の増加、約1.8倍の増加~約4.5倍の増加、約1.8倍の増加~約4.0倍の増加、約1.8倍の増加~約3.5倍の増加、約1.8倍の増加~約3.0倍の増加、約1.8倍の増加~約2.8倍の増加、約1.8倍の増加~約2.6倍の増加、約1.8倍の増加~約2.5倍の増加、約1.8倍の増加~約2.4倍の増加、約1.8倍の増加~約2.2倍の増加、約1.8倍の増加~約2.0倍の増加、約2.0倍の増加~約100倍の増加、約2.0倍の増加~約90倍の増加、約2.0倍の増加~約80倍の増加、約2.0倍の増加~約70倍の増加、約2.0倍の増加~約60倍の増加、約2.0倍の増加~約50倍の増加、約2.0倍の増加~約40倍の増加、約2.0倍の増加~約30倍の増加、約2.0倍の増加~約20倍の増加、約2.0倍の増加~約10倍の増加、約2.0倍の増加~約9.5倍の増加、約2.0倍の増加~約9.0倍の増加、約2.0倍の増加~約8.5倍の増加、約2.0倍の増加~約8.0倍の増加、約2.0倍の増加~約7.5倍の増加、約2.0倍の増加~約7.0倍の増加、約2.0倍の増加~約6.5倍の増加、約2.0倍の増加~約6.0倍の増加、約2.0倍の増加~約5.5倍の増加、約2.0倍の増加~約5.0倍の増加、約2.0倍の増加~約4.5倍の増加、約2.0倍の増加~約4.0倍の増加、約2.0倍の増加~約3.5倍の増加、約2.0倍の増加~約3.0倍の増加、約2.0倍の増加~約2.8倍の増加、約2.0倍の増加~約2.6倍の増加、約2.0倍の増加~約2.5倍の増加、約2.0倍の増加~約2.4倍の増加、約2.0倍の増加~約2.2倍の増加、約2.2倍の増加~約100倍の増加、約2.2倍の増加~約90倍の増加、約2.2倍の増加~約80倍の増加、約2.2倍の増加~約70倍の増加、約2.2倍の増加~約60倍の増加、約2.2倍の増加~約50倍の増加、約2.2倍の増加~約40倍の増加、約2.2倍の増加~約30倍の増加、約2.2倍の増加~約20倍の増加、約2.2倍の増加~約10倍の増加、約2.2倍の増加~約9.5倍の増加、約2.2倍の増加~約9.0倍の増加、約2.2倍の増加~約8.5倍の増加、約2.2倍の増加~約8.0倍の増加、約2.2倍の増加~約7.5倍の増加、約2.2倍の増加~約7.0倍の増加、約2.2倍の増加~約6.5倍の増加、約2.2倍の増加~約6.0倍の増加、約2.2倍の増加~約5.5倍の増加、約2.2倍の増加~約5.0倍の増加、約2.2倍の増加~
約4.5倍の増加、約2.2倍の増加~約4.0倍の増加、約2.2倍の増加~約3.5倍の増加、約2.2倍の増加~約3.0倍の増加、約2.2倍の増加~約2.8倍の増加、約2.2倍の増加~約2.6倍の増加、約2.2倍の増加~約2.5倍の増加、約2.2倍の増加~約2.4倍の増加、約2.4倍の増加~約100倍の増加、約2.4倍の増加~約90倍の増加、約2.4倍の増加~約80倍の増加、約2.4倍の増加~約70倍の増加、約2.4倍の増加~約60倍の増加、約2.4倍の増加~約50倍の増加、約2.4倍の増加~約40倍の増加、約2.4倍の増加~約30倍の増加、約2.4倍の増加~約20倍の増加、約2.4倍の増加~約10倍の増加、約2.4倍の増加~約9.5倍の増加、約2.4倍の増加~約9.0倍の増加、約2.4倍の増加~約8.5倍の増加、約2.4倍の増加~約8.0倍の増加、約2.4倍の増加~約7.5倍の増加、約2.4倍の増加~約7.0倍の増加、約2.4倍の増加~約6.5倍の増加、約2.4倍の増加~約6.0倍の増加、約2.4倍の増加~約5.5倍の増加、約2.4倍の増加~約5.0倍の増加、約2.4倍の増加~約4.5倍の増加、約2.4倍の増加~約4.0倍の増加、約2.4倍の増加~約3.5倍の増加、約2.4倍の増加~約3.0倍の増加、約2.4倍の増加~約2.8倍の増加、約2.4倍の増加~約2.6倍の増加、約2.6倍の増加~約100倍の増加、約2.6倍の増加~約90倍の増加、約2.6倍の増加~約80倍の増加、約2.6倍の増加~約70倍の増加、約2.6倍の増加~約60倍の増加、約2.6倍の増加~約50倍の増加、約2.6倍の増加~約40倍の増加、約2.6倍の増加~約30倍の増加、約2.6倍の増加~約20倍の増加、約2.6倍の増加~約10倍の増加、約2.6倍の増加~約9.5倍の増加、約2.6倍の増加~約9.0倍の増加、約2.6倍の増加~約8.5倍の増加、約2.6倍の増加~約8.0倍の増加、約2.6倍の増加~約7.5倍の増加、約2.6倍の増加~約7.0倍の増加、約2.6倍の増加~約6.5倍の増加、約2.6倍の増加~約6.0倍の増加、約2.6倍の増加~約5.5倍の増加、約2.6倍の増加~約5.0倍の増加、約2.6倍の増加~約4.5倍の増加、約2.6倍の増加~約4.0倍の増加、約2.6倍の増加~約3.5倍の増加、約2.6倍の増加~約3.0倍の増加、約2.6倍の増加~約2.8倍の増加、約2.8倍の増加~約100倍の増加、約2.8倍の増加~約90倍の増加、約2.8倍の増加~約80倍の増加、約2.8倍の増加~約70倍の増加、約2.8倍の増加~約60倍の増加、約2.8倍の増加~約50倍の増加、約2.8倍の増加~約40倍の増加、約2.8倍の増加~約30倍の増加、約2.8倍の増加~約20倍の増加、約2.8倍の増加~約10倍の増加、約2.8倍の増加~約9.5倍の増加、約2.8倍の増加~約9.0倍の増加、約2.8倍の増加~約8.5倍の増加、約2.8倍の増加~約8.0倍の増加、約2.8倍の増加~約7.5倍の増加、約2.8倍の増加~約7.0倍の増加、約2.8倍の増加~約6.5倍の増加、約2.8倍の増加~約6.0倍の増加、約2.8倍の増加~約5.5倍の増加、約2.8倍の増加~約5.0倍の増加、約2.8倍の増加~約4.5倍の増加、約2.8倍の増加~約4.0倍の増加、約2.8倍の増加~約3.5倍の増加、約2.8倍の増加~約3.0倍の増加、約3.0倍の増加~約100倍の増加、約3.0倍の増加~約90倍の増加、約3.0倍の増加~約80倍の増加、約3.0倍の増加~約70倍の増加、約3.0倍の増加~約60倍の増加、約3.0倍の増加~約50倍の増加、約3.0倍の増加~約40倍の増加、約3.0倍の増加~約30倍の増加、約3.0倍の増加~約20倍の増加、約3.0倍の増加~約10倍の増加、約3.0倍の増加~約9.5倍の増加、約3.0倍の増加~約9.0倍の増加、約3.0倍の増加~約8.5倍の増加、約3.0倍の増加~約8.0倍の増加、約3.0倍の増加~約7.5倍の増加、約3.0倍の増加~約7.0倍の増加、約3.0倍の増加~約6.5倍の増加、約3.0倍の増加~約6.0倍の増加、約3.0倍の増加~約5.5倍の増加、約3.0倍の増加~約5.0倍の増加、約3.0倍の増加~約4.5倍の増加、約3.0倍の増加~約4.0倍の増加、約3.0倍の増加~約3.5倍の増加、約3.5倍の増加~約100倍の増加、約3.5倍の増加~約90倍の増加、約3.5倍の増加~約80倍の増加、約3.5倍の増加~約70倍の増加、約3.5倍の増加~約60倍の増加、約3.5倍の増加~約50倍の増加、約3.5倍の増加~約40倍の増加、約3.5倍の増加~約30倍の増加、約3.5倍の増加~約20倍の増加、約3.5倍の増加~約10倍の増加、約3.5倍の増加~約9.5倍の増加、約3.5倍の増加~約9.0倍の増加、約3.5倍の増加~約8.5倍の増加、約3.5倍の増加~約8.0倍の増加、約3.5倍の増加~約7.5倍の増加、約3.5倍の増加~約7.0倍の増加、約3.5倍の増加~約6.5倍の増加、約3.5倍の増加~約6.0倍の増加、約3.5倍の増加~約5.5倍の増加、約3.5倍の増加~約5.0倍の増加、約3.5倍の増加~約4.5倍の増加、約3.5倍の増加~約4.0倍の増加、約4.0倍の増加~約100倍の増加、約4.0倍の増加~約90倍の増加、約4.0倍の増加~約80倍の増加、約4.0倍の増加~約70倍の増加、約4.0倍の増加~約60倍の増加、約4.0倍の増加~約50倍の増加、約4.0倍の増加~約40倍の増加、約4.0倍の増加~約30倍の増加、約4.0倍の増加~約20倍の増加、約4.0倍の増加~約10倍の増加、約4.0倍の増加~約9.5倍の増加、約4.0倍の増加~約9.0倍の増加、約4.0倍の増加~約8.5倍の増加、約4.0倍の増加~約8.0倍の増加、約4.0倍の増加~約7.5倍の増加、約4.0倍の増加~約7.0倍の増加、約4.0倍の増加~約6.5倍の増加、約4.0倍の増加~約6.0倍の増加、約4.0倍の増加~約5.5倍の増加、約4.0倍の増加~約5.0倍の増加、約4.0倍の増加~約4.5倍の増加、約4.5倍の増加~約100倍の増加、約4.5倍の増加~約90倍の増加、約4.5倍の増加~約80倍の増加、約4.5倍の増加~約70倍の増加、約4.5倍の増加~約60倍の増加、約4.5倍の増加~約50倍の増加、約4.5倍の増加~約40倍の増加、約4.5倍の増加~約30倍の増加、約4.5倍の増加~約20倍の増加、約4.5倍の増加~約10倍の増加、約4.5倍の増加~約9.5倍の増加、約4.5倍の増加~約9.0倍の増加、約4.5倍の増加~約8.5倍の増加、約4.5倍の増加~約8.0倍の増加、約4.5倍の増加~約7.5倍の増加、約4.5倍の増加~約7.0倍の増加、約4.5倍の増加~約6.5倍の増加、約4.5倍の増加~約6.0倍の増加、約4.5倍の増加~約5.5倍の増加、約4.5倍の増加~約5.0倍の増加、約5.0倍の増加~約100倍の増加、約5.0倍の増加~約90倍の増加、約5.0倍の増加~約80倍の増加、約5.0倍の増加~約70倍の増加、約5.0倍の増加~約60倍の増加、約5.0倍の増加~約50倍の増加、約5.0倍の増加~約40倍の増加、約5.0倍の増加~約30倍の増加、約5.0倍の増加~約20倍の増加、約5.0倍の増加~約10倍の増加、約5.0倍の増加~約9.5倍の増加、約5.0倍の増加~約9.0倍の増加、約5.0倍の増加~約8.5倍の増加、約5.0倍の増加~約8.0倍の増加、約5.0倍の増加~約7.5倍の増加、約5.0倍の増加~約7.0倍の増加、約5.0倍の増加~約6.5倍の増加、約5.0倍の増加~約6.0倍の増加、約5.0倍の増加~約5.5倍の増加、約5.5倍の増加~約100倍の増加、約5.5倍の増加~約90倍の増加、約5.5倍の増加~約80倍の増加、約5.5倍の増加~約70倍の増加、約5.5倍の増加~約60倍の増加、約5.5倍の増加~約50倍の増加、約5.5倍の増加~約40倍の増加、約5.5倍の増加~約30倍の増加、約5.5倍の増加~約20倍の増加、約5.5倍の増加~約10倍の増加、約5.5倍の増加~約9.5倍の増加、約5.5倍の増加~約9.0倍の増加、約5.5倍の増加~約8.5倍の増加、約5.5倍の増加~約8.0倍の増加、約5.5倍の増加~約7.5倍の増加、約5.5倍の増加~約7.0倍の増加、約5.5倍の増加~約6.5倍の増加、約5.5倍の増加~約6.0倍の増加、約6.0倍の増加~約100倍の増加、約6.0倍の増加~約90倍の増加、約6.0倍の増加~約80倍の増加、約6.0倍の増加~約70倍の増加、約6.0倍の増加~約60倍の増加、約6.0倍の増加~約50倍の増加、約6.0倍の増加~約40倍の増加、約6.0倍の増加~約30倍の増加、約6.0倍の増加~約20倍の増加、約6.0倍の増加~約10倍の増加、約6.0倍の増加~約9.5倍の増加、約6.0倍の増加~約9.0倍の増加、約6.0倍の増加~約8.5倍の増加、約6.0倍の増加~約8.0倍の増加、約6.0倍の増加~約7.5倍の増加、約6.0倍の増加~約7.0倍の増加、約6.0倍の増加~約6.5倍の増加、約6.5倍の増加~約100倍の増加、約6.5倍の増加~約90倍の増加、約6.5倍の増加~約80倍の増加、約6.5倍の増加~約70倍の増加、約6.5倍の増加~約60倍の増加、約6.5倍の増加~約50倍の増加、約6.5倍の増加~約40倍の増加、約6.5倍の増加~約30倍の増加、約6.5倍の増加~約20倍の増加、約6.5倍の増加~約10倍の増加、約6.5倍の増加~約9.5倍の増加、約6.5倍の増加~約9.0倍の増加、約6.5倍の増加~約8.5倍の増加、約6.5倍の増加~約8.0倍の増加、約6.5倍の増加~約7.5倍の増加、約6.5倍の増加~約7.0倍の増加、約7.0倍の増加~約100倍の増加、約7.0倍の増加~約90倍の増加、約7.0倍の増加~約80倍の増加、約7.0倍の増加~約70倍の増加、約7.0倍の増加~約60倍の増加、約7.0倍の増加~約50倍の増加、約7.0倍の増加~約40倍の増加、約7.0倍の増加~約30倍の増加、約7.0倍の増加~約20倍の増加、約7.0倍の増加~約10倍の増加、約7.0倍の増加~約9.5倍の増加、約7.0倍の増加~約9.0倍の増加、約7.0倍の増加~約8.5倍の増加、約7.0倍の増加~約8.0倍の増加、約7.0倍の増加~約7.5倍の増加、約7.5倍の増加~約100倍の増加、約7.5倍の増加~約90倍の増加、約7.5倍の増加~約80倍の増加、約7.5倍の増加~約70倍の増加、約7.5倍の増加~約60倍の増加、約7.5倍の増加~約50倍の増加、約7.5倍の増加~約40倍の増加、約7.5倍の増加~約30倍の増加、約7.5倍の増加~約20倍の増加、約7.5倍の増加~約10倍の増加、約7.5倍の増加~約9.5倍の増加、約7.5倍の増加~約9.0倍の増加、約7.5倍の増加~約8.5倍の増加、約7.5倍の増加~約8.0倍の増加、約8.0倍の増加~約100倍の増加、約8.0倍の増加~約90倍の増加、約8.0倍の増加~約80倍の増加、約8.0倍の増加~約70倍の増加、約8.0倍の増加~約60倍の増加、約8.0倍の増加~約50倍の増加、約8.0倍の増加~約40倍の増加、約8.0倍の増加~約30倍の増加、約8.0倍の増加~約20倍の増加、約8.0倍の増加~約10倍の増加、約8.0倍の増加~約9.5倍の増加、約8.0倍の増加~約9.0倍の増加、約8.0倍の増加~約8.5倍の増加、約8.5倍の増加~約100倍の増加、約8.5倍の増加~約90倍の増加、約8.5倍の増加~約80倍の増加、約8.5倍の増加~約70倍の増加、約8.5倍の増加~約60倍の増加、約8.5倍の増加~約50倍の増加、約8.5倍の増加~約40倍の増加、約8.5倍の増加~約30倍の増加、約8.5倍の増加~約20倍の増加、約8.5倍の増加~約10倍の増加、約8.5倍の増加~約9.5倍の増加、約8.5倍の増加~
約9.0倍の増加、約9.0倍の増加~約100倍の増加、約9.0倍の増加~約90倍の増加、約9.0倍の増加~約80倍の増加、約9.0倍の増加~約70倍の増加、約9.0倍の増加~約60倍の増加、約9.0倍の増加~約50倍の増加、約9.0倍の増加~約40倍の増加、約9.0倍の増加~約30倍の増加、約9.0倍の増加~約20倍の増加、約9.0倍の増加~約10倍の増加、約9.0倍の増加~約9.5倍の増加、約9.5倍の増加~約100倍の増加、約9.5倍の増加~約90倍の増加、約9.5倍の増加~約80倍の増加、約9.5倍の増加~約70倍の増加、約9.5倍の増加~約60倍の増加、約9.5倍の増加~約50倍の増加、約9.5倍の増加~約40倍の増加、約9.5倍の増加~約30倍の増加、約9.5倍の増加~約20倍の増加、約9.5倍の増加~約10倍の増加、約10倍の増加~約100倍の増加、約10倍の増加~約90倍の増加、約10倍の増加~約80倍の増加、約10倍の増加~約70倍の増加、約10倍の増加~約60倍の増加、約10倍の増加~約50倍の増加、約10倍の増加~約40倍の増加、約10倍の増加~約30倍の増加、約10倍の増加~約20倍の増加、約20倍の増加~約100倍の増加、約20倍の増加~約90倍の増加、約20倍の増加~約80倍の増加、約20倍の増加~約70倍の増加、約20倍の増加~約60倍の増加、約20倍の増加~約50倍の増加、約20倍の増加~約40倍の増加、約20倍の増加~約30倍の増加、約30倍の倍増~約100倍の増加、約30倍の増加~約90倍の増加、約30倍の増加~約80倍の増加、約30倍の増加~約70倍の増加、約30倍の増加~約60倍の増加、約30倍の増加~約50倍の増加、約30倍の増加~約40倍の増加、約40倍の増加~約100倍の増加、約40倍の増加~約90倍の増加、約40倍の増加~約80倍の増加、約40倍の増加~約70倍の増加、約40倍の増加~約60倍の増加、約40倍の増加~約50倍の増加、約50倍の増加~約100倍の増加、約50倍の増加~約90倍の増加、約50倍の増加~約80倍の増加、約50倍の増加~約70倍の増加、約50倍の増加~約60倍の増加、約60倍の増加~約100倍の増加、約60倍の増加~約90倍の増加、約60倍の増加~約80倍の増加、約60倍の増加~約70倍の増加、約70倍の増加~約100倍の増加、約70倍の増加~約90倍の増加、約70倍の増加~約80倍の増加、約80倍の増加~約100倍の増加、約80倍の増加~約90倍の増加、または約90倍の増加~約100倍の増加)を提供することができる。
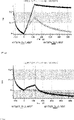
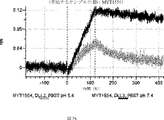
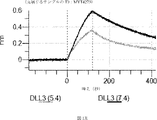
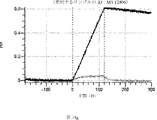
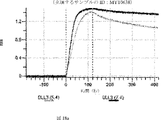
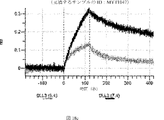
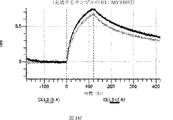
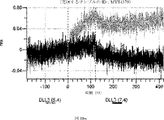
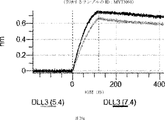
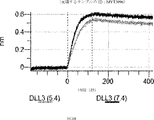
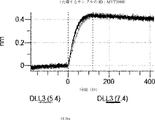
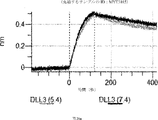
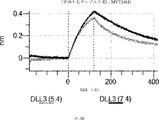
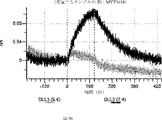
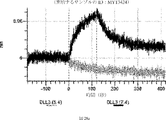
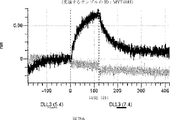
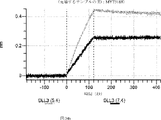
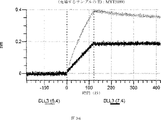
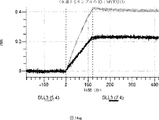
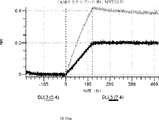
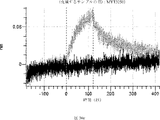
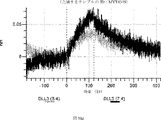
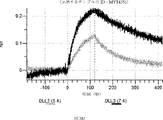
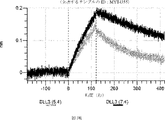
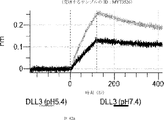
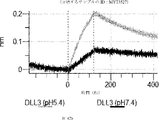
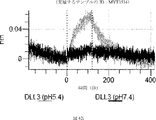
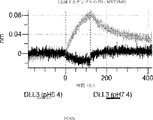
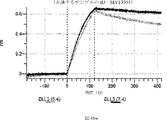
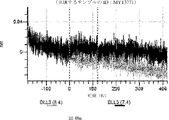
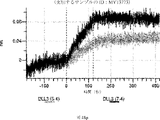
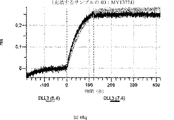
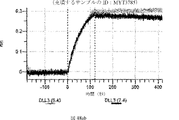
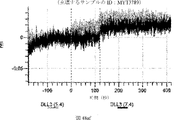
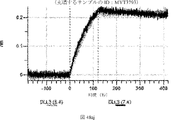
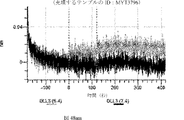
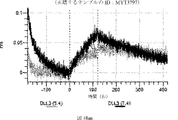
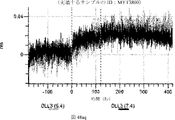
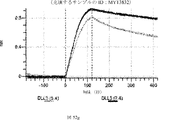
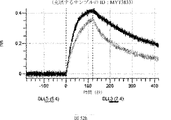
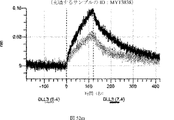
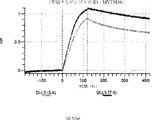
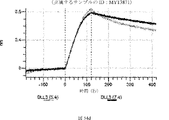
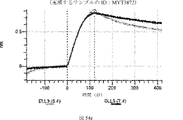
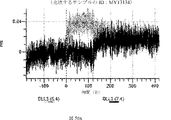
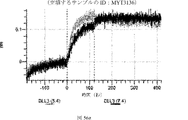
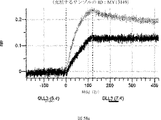
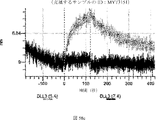
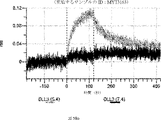
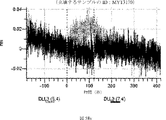
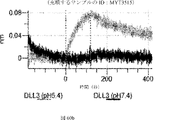
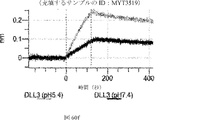
デルタ様3(DLL3)は、当該技術分野で知られている腫瘍抗原であり、腫瘍学における治療用抗体の標的である(Saunders LRら(2015)”A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo.Science Translational Medicine 7(302):302ra136を参照)。成熟ヒトDLL3の配列は、配列番号9に見出すことができる。成熟ヒトDLL3をコードするcDNAの配列は、配列番号10に見出すことができる。DLL3の細胞外ドメインの配列は、配列番号11に見出すことができる。DLL3の細胞外ドメインをコードするcDNAの配列は、配列番号12に見出すことができる。
本明細書に記載の抗原結合タンパク質構築物(ABPC)のいずれも、単一のポリペプチドであり得るか、または2、3、4、5、6、7、8、9、もしくは10個(同一または異なる)のポリペプチドを含むことができる。ABPCが単一のポリペプチドであるいくつかの実施形態では、ABPCは、単一の抗原結合ドメインまたは2つの抗原結合ドメインを含むことができる。ABPCが単一のポリペプチドであり、2つの抗原結合ドメインを含むいくつかの実施形態では、第1および第2の抗原結合ドメインは、互いに同一であっても異なることができる(同じまたは異なる抗原またはエピトープに特異的に結合することができる)。
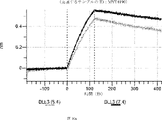
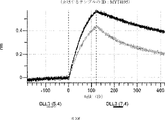
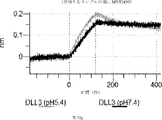
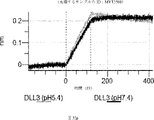
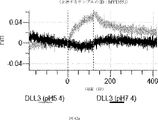
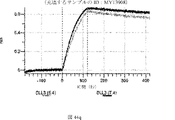
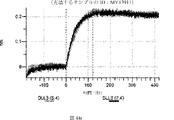
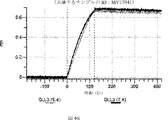
本明細書に記載の抗原結合タンパク質構築物(ABPC)のいずれかのいくつかの実施形態では、約4.0~約6.5(例えば、約4.0~約6.4、約4.0~約6.3、約4.0~約6.2、約4.0~約6.1、約4.0~約6.0、約4.0~約5.9、約4.0~約5.8、約4.0~約5.7、約4.0~約5.6、約4.0~約5.5、約4.0~約5.4、約4.0~約5.3、約4.0~約5.2、約4.0~約5.1、約4.0~約5.0、約4.0~約4.9、約4.0~約4.8、約4.0~約4.7、約4.0~約4.6、約4.0~約4.5、約4.0~約4.4、約4.0~約4.3、約4.0~約4.2、約4.0~約4.1、約4.1~約6.5、約4.1~約6.4、約4.1~約6.3、約4.1~約6.2、約4.1~約6.1、約4.1~約6.0、約4.1~約5.9、約4.1~約5.8、約4.1~約5.7、約4.1~約5.6、約4.1~約5.5、約4.1~約5.4、約4.1~約5.3、約4.1~約5.2、約4.1~約5.1、約4.1~約5.0、約4.1~約4.9、約4.1~約4.8、約4.1~約4.7、約4.1~約4.6、約4.1~約4.5、約4.1~約4.4、約4.1~約4.3、約4.1~約4.2、約4.2~約6.5、約4.2~約6.4、約4.2~約6.3、約4.2~約6.2、約4.2~約6.1、約4.2~約6.0、約4.2~約5.9、約4.2~約5.8、約4.2~約5.7、約4.2~約5.6、約4.2~約5.5、約4.2~約5.4、約4.2~約5.3、約4.2~約5.2、約4.2~約5.1、約4.2~約5.0、約4.2~約4.9、約4.2~約4.8、約4.2~約4.7、約4.2~約4.6、約4.2~約4.5、約4.2~約4.4、約4.2~約4.3、約4.3~約6.5、約4.3~約6.4、約4.3~約6.3、約4.3~約6.2、約4.3~約6.1、約4.3~約6.0、約4.3~約5.9、約4.3~約5.8、約4.3~約5.7、約4.3~約5.6、約4.3~約5.5、約4.3~約5.4、約4.3~約5.3、約4.3~約5.2、約4.3~約5.1、約4.3~約5.0、約4.3~約4.9、約4.3~約4.8、約4.3~約4.7、約4.3~約4.6、約4.3~約4.5、約4.3~約4.4、約4.4~約6.5、約4.4~約6.4、約4.4~約6.3、約4.4~約6.2、約4.4~約6.1、約4.4~約6.0、約4.4~約5.9、約4.4~約5.8、約4.4~約5.7、約4.4~約5.6、約4.4~約5.5、約4.4~約5.4、約4.4~約5.3、約4.4~約5.2、約4.4~約5.1、約4.4~約5.0、約4.4~約4.9、約4.4~約4.8、約4.4~約4.7、約4.4~約4.6、約4.4~約4.5、約4.5~約6.5、約4.5~約6.4、約4.5~約6.3、約4.5~約6.2、約4.5~約6.1、約4.5~約6.0、約4.5~約5.9、約4.5~約5.8、約4.5~約5.7、約4.5~約5.6、約4.5~約5.5、約4.5~約5.4、約4.5~約5.3、約4.5~約5.2、約4.5~約5.1、約4.5~約5.0、約4.5~約4.9、約4.5~約4.8、約4.5~約4.7、約4.5~約4.6、約4.6~約6.5、約4.6~約6.4、約4.6~約6.3、約4.6~約6.2、約4.6~約6.1、約4.6~約6.0、約4.6~約5.9、約4.6~約5.8、約4.6~約5.7、約4.6~約5.6、約4.6~約5.5、約4.6~約5.4、約4.6~約5.3、約4.6~約5.2、約4.6~約5.1、約4.6~約5.0、約4.6~約4.9、約4.6~約4.8、約4.6~約4.7、約4.7~約6.5、約4.7~約6.4、約4.7~約6.3、約4.7~約6.2、約4.7~約6.1、約4.7~約6.0、約4.7~約5.9、約4.7~約5.8、約4.7~約5.7、約4.7~約5.6、約4.7~約5.5、約4.7~約5.4、約4.7~約5.3、約4.7~約5.2、約4.7~約5.1、約4.7~約5.0、約4.7~約4.9、約4.7~約4.8、約4.8~約6.5、約4.8~約6.4、約4.8~約6.3、約4.8~約6.2、約4.8~約6.1、約4.8~約6.0、約4.8~約5.9、約4.8~約5.8、約4.8~約5.7、約4.8~約5.6、約4.8~約5.5、約4.8~約5.4、約4.8~約5.3、約4.8~約5.2、約4.8~約5.1、約4.8~約5.0、約4.8~約4.9、約4.9~約6.5、約4.9~約6.4、約4.9~約6.3、約4.9~約6.2、約4.9~約6.1、約4.9~約6.0、約4.9~約5.9、約4.9~約5.8、約4.9~約5.7、約4.9~約5.6、約4.9~約5.5、約4.9~約5.4、約4.9~約5.3、約4.9~約5.2、約4.9~約5.1、約4.9~約5.0、約5.0~約6.5、約5.0~約6.4、約5.0~約6.3、約5.0~約6.2、約5.0~約6.1、約5.0~約6.0、約5.0~約5.9、約5.0~約5.8、約5.0~約5.7、約5.0~約5.6、約5.0~約5.5、約5.0~約5.4、約5.0~約5.3、約5.0~約5.2、約5.0~約5.1、約5.1~約6.5、約5.1~約6.4、約5.1~約6.3、約5.1~約6.2、約5.1~約6.1、約5.1~約6.0、約5.1~約5.9、約5.1~約5.8、約5.1~約5.7、約5.1~約5.6、約5.1~約5.5、約5.1~約5.4、約5.1~約5.3、約5.1~約5.2、約5.2~約6.5、約5.2~約6.4、約5.2~約6.3、約5.2~約6.2、約5.2~約6.1、約5.2~約6.0、約5.2~約5.9、約5.2~約5.8、約5.2~約5.7、約5.2~約5.6、約5.2~約5.5、約5.2~約5.4、約5.2~約5.3、約5.3~約6.5、約5.3~約6.4、約5.3~約6.3、約5.3~約6.2、約5.3~約6.1、約5.3~約6.0、約5.5~約5.9、約5.3~約5.8、約5.3~約5.7、約5.3~約5.6、約5.3~約5.5、約5.3~約5.4、約5.4~約6.5、約5.4~約6.4、約5.4~約6.3、約5.4~約6.2、約5.4~約6.1、約5.4~約6.0、約5.4~約5.9、約5.4~約5.8、約5.4~約5.7、約5.4~約5.6、約5.4~約5.5、約5.5~約6.5、約5.5~約6.4、約5.5~約6.3、約5.5~約6.2、約5.5~約6.1、約5.5~約6.0、約5.5~約5.9、約5.5~約5.8、約5.5~約5.7、約5.5~約5.6、約5.6~約6.5、約5.6~約6.4、約5.6~約6.3、約5.6~約6.2、約5.6~約6.1、約5.6~約6.0、約5.6~約5.9、約5.6~約5.8、約5.6~約5.7、約5.7~約6.5、約5.7~約6.4、約5.7~約6.3、約5.7~約6.2、約5.7~約6.1、約5.7~約6.0、約5.7~約5.9、約5.7~約5.8、約5.8~約6.5、約5.8~約6.4、約5.8~約6.3、約5.8~約6.2、約5.8~約6.1、約5.8~約6.0、約5.8~約5.9、約5.9~約6.5、約5.9~約6.4、約5.9~約6.3、約5.9~約6.2、約5.9~約6.1、約5.9~約6.0、約6.0~約6.5、約6.0~約6.4、約6.0~約6.3、約6.0~約6.2、約6.0~約6.1、約6.1~約6.5、約6.1~約6.4、約6.1~約6.3、約6.1~約6.2、約6.2~約6.5、約6.2~約6.4、約6.2~約6.3、約6.3~約6.5、約6.3~約6.4、または約6.4~約6.5)のpHでの第1の抗原結合ドメイン(および場合により第2の抗原結合ドメイン(存在する場合))の解離速度は、約7.0から約8.0(例えば、(例えば、約7.0~約7.9、約7.0~約7.8、約7.0~約7.7、約7.0~約7.6、約7.0~約7.5、約7.0~約7.4、約7.0~約7.3、約7.0~約7.2、約7.0~約7.1、約7.1~約8.0、約7.1~約7.9、約7.1~約7.8、約7.1~約7.7、約7.1~約7.6、約7.1~約7.5、約7.1~約7.4、約7.1~約7.3、約7.1~約7.2、約7.2~約8.0、約7.2~約7.9、約7.2~約7.8、約7.2~約7.7、約7.2~約7.6、約7.2~約7.5、約7.2~約7.4、約7.2~約7.3、約7.3~約8.0、約7.3~約7.9、約7.3~約7.8、約7.3~約7.7、約7.3~約7.6、約7.3~約7.5、約7.3~約7.4、約7.4~約8.0、約7.4~約7.9、約7.4~約7.8、約7.4~約7.7、約7.4~約7.6、約7.4~約7.5、約7.5~約8.0、約7.5~約7.9、約7.5~約7.8、約7.5~約7.7、約7.5~約7.6、約7.6~約8.0、約7.6~約7.9、約7.6~約7.8、約7.6~約7.7、約7.7~約8.0、約7.7~約7.9、約7.7~約7.8、約7.8~約8.0、約7.8~約7.9、または約7.9~約8.0)のpHでの解離速度よりも速い(たとえば、少なくとも5%より速く、少なくとも10%より速く、少なくとも15%より速く、少なくとも20%、少なくとも25%より速く、少なくとも30%より速く、少なくとも35%より速く、少なくとも40%より速く、少なくとも45%より速く、少なくとも50%より速く、少なくとも55%より速く、少なくとも60%より速く、少なくとも65%より速く、少なくとも70%より速く、少なくとも75%より速く、少なくとも80%より速く、少なくとも85%より速く、少なくとも90%より速く、少なくとも95%より速く、少なくとも100%より速く、少なくとも120%より速く、少なくとも140%より速く、少なくとも160%より速く、少なくとも180%より速く、少なくとも200%より速く、少なくとも220%より速く、少なくとも240%より速く、少なくとも260%より速く、少なくとも280%より速く、少なくとも300%より速く、少なくとも320%より速く、少なくとも340%より速く、少なくとも360%より速く、少なくとも380%より速く、少なくとも400%より速く少なくとも420%より速く少なくとも440%より速く少なくとも460%より速く少なくとも480%より速く、少なくとも500%より速く、少なくとも1,000%より速く、少なくとも2,000%より速く、少なくとも3,000%より速く、少なくとも4,000%より速く、少なくとも5,000%、少なくとも6,000%より速く、少なくとも7,000%より速く、少なくとも8,000%より速く、少なくとも9,000%より速く、または少なくとも10,000%より速く、または約5%より速く~約10,000%より速く、約5%より速く~約9,000%より速く、約5%より速く~約8,000%より速く、約5%より速く~約7,000%より速く、約5%より速く~約6,000%より速く、約5%より速く~約5,000%より速く、約5%より速く~約4,000%より速く、約5%より速く~約3,000%より速く、約5%より速く~約2,000%より速く、約5%より速く~約1,000%より速く、約5%より速く~約500%より速く、約5%より速く~約480%より速く、約5%より速く~約460%より速く、約5%より速く~約440%より速く、約5%より速く~約420%より速く、約5%より速く~約400%より速く、約5%より速く~約380%より速く、約5%より速く~約360%より速く、約5%より速く~約340%より速く、約5%より速く~約320%より速く、約5%より速く~約300%より速く、約5%より速く~約280%より速く、約5%より速く~約260%より速く、約5%より速く~約240%より速く、約5%より速く~約220%より速く、約5%より速く~約200%より速く、
約5%より速く~約180%より速く、約5%より速く~約160%より速く、約5%より速く~約140%より速く、約5%より速く~約120%より速く、約5%より速く~約100%より速く、約5%より速く~約95%より速く、約5%より速く~約90%より速く、約5%より速く~約85%より速く、約5%より速く~約80%より速く、約5%より速く~約75%より速く、約5%より速く~約70%より速く、約5%より速く~約65%より速く、約5%より速く~約60%より速く、約5%より速く~約55%より速く、約5%より速く~約50%より速く、約5%より速く~約45%より速く、約5%より速く~約40%より速く、約5%より速く~約35%より速く、約5%より速く~約30%より速く、約5%より速く~約25%より速く、約5%より速く~約20%より速く、約5%より速く~約15%より速く、約5%より速く~約10%より速く、約10%より速く~約10,000%より速く、約10%より速く~約9,000%より速く、約10%より速く~約8,000%より速く、約10%より速く~約7,000%より速く、約10%より速く~約6,000%より速く、約10%より速く~約5,000%より速く、約10%より速く~約4,000%より速く、約10%より速く~約3,000%より速く、約10%より速く~約2,000%より速く、約10%より速く~約1,000%より速く、約10%より速く~約500%より速く、約10%より速く~約480%より速く、約10%より速く~約460%より速く、約10%より速く~約440%より速く、約10%より速く~約420%より速く、約10%より速く~約400%より速く、約10%より速く~約380%より速く、約10%より速く~約360%より速く、約10%より速く~約340%より速く、約10%より速く~約320%より速く、約10%より速く~約300%より速く、約10%より速く~約280%より速く、約10%より速く~約260%より速く、約10%より速く~約240%より速く、約10%より速く~約220%より速く、約10%より速く~約200%より速く、約10%より速く~約180%より速く、約10%より速く~約160%より速く、約10%より速く~約140%より速く、約10%より速く~約120%より速く、約10%より速く~約100%より速く、約10%より速く~約95%より速く、約10%より速く~約90%より速く、約10%より速く~約85%より速く、約10%より速く~約80%より速く、約10%より速く~約75%より速く、約10%より速く~約70%より速く、約10%より速く~約65%より速く、約10%より速く~約60%より速く、約10%より速く~約55%より速く、約10%より速く~約50%より速く、約10%より速く~約45%より速く、約10%より速く~約40%より速く、約10%より速く~約35%より速く、約10%より速く~約30%より速く、約10%より速く~約25%より速く、約10%より速く~約20%より速く、約10%より速く~約15%より速く、約15%より速く~約10,000%より速く、約15%より速く~約9,000%より速く、約15%より速く~約8,000%より速く、約15%より速く~約7,000%より速く、約15%より速く~約6,000%より速く、約15%より速く~約5,000%より速く、約15%より速く~約4,000%より速く、約15%より速く~約3,000%より速く、約15%より速く~約2,000%より速く、約15%より速く~約1,000%より速く、約15%より速く~約500%より速く、約15%より速く~約480%より速く、約15%より速く~約460%より速く、約15%より速く~約440%より速く、約15%より速く~約420%より速く、約15%より速く~約400%より速く、約15%より速く~約380%より速く、約15%より速く~約360%より速く、約15%より速く~約340%より速く、約15%より速く~約320%より速く、約15%より速く~約300%より速く、約15%より速く~約280%より速く、約15%より速く~約260%より速く、約15%より速く~約240%より速く、約15%より速く~約220%より速く、約15%より速く~約200%より速く、約15%より速く~約180%より速く、約15%より速く~約160%より速く、約15%より速く~約140%より速く、約15%より速く~約120%より速く、約15%より速く~約100%より速く、約15%より速く~約95%より速く、約15%より速く~約90%より速く、約15%より速く~約85%より速く、約15%より速く~約80%より速く、約15%より速く~約75%より速く、約15%より速く~約70%より速く、約15%より速く~約65%より速く、約15%より速く~約60%より速く、約15%より速く~約55%より速く、約15%より速く~約50%より速く、約15%より速く~約45%より速く、約15%より速く~約40%より速く、約15%より速く~約35%より速く、約15%より速く~約30%より速く、約15%より速く~約25%より速く、約15%より速く~約20%より速く、約20%より速く~約10,000%より速く、約20%より速く~約9,000%より速く、約20%より速く~約8,000%より速く、約20%より速く~約7,000%より速く、約20%より速く~約6,000%より速く、約20%より速く~約5,000%より速く、約20%より速く~約4,000%より速く、約20%より速く~約3,000%より速く、約20%より速く~約2,000%より速く、約20%より速く~約1,000%より速く、約20%より速く~約500%より速く、約20%より速く~約480%より速く、約20%より速く~約460%より速く、約20%より速く~約440%より速く、約20%より速く~約420%より速く、約20%より速く~約400%より速く、約20%より速く~約380%より速く、約20%より速く~約360%より速く、約20%より速く~約340%より速く、約20%より速く~約320%より速く、約20%より速く~約300%より速く、約20%より速く~約280%より速く、約20%より速く~約260%より速く、約20%より速く~約240%より速く、約20%より速く~約220%より速く、約20%より速く~約200%より速く、約20%より速く~約180%より速く、約20%より速く~約160%より速く、約20%より速く~約140%より速く、約20%より速く~約120%より速く、約20%より速く~約100%より速く、約20%より速く~約95%より速く、約20%より速く~約90%より速く、約20%より速く~約85%より速く、約20%より速く~約80%より速く、約20%より速く~約75%より速く、約20%より速く~約70%より速く、約20%より速く~約65%より速く、約20%より速く~約60%より速く、約20%より速く~約55%より速く、約20%より速く~約50%より速く、約20%より速く~約45%より速く、約20%より速く~約40%より速く、約20%より速く~約35%より速く、約20%より速く~約30%より速く、約20%より速く~約25%より速く、約25%より速く~約10,000%より速く、約25%より速く~約9,000%より速く、約25%より速く~約8,000%より速く、約25%より速く~約7,000%より速く、約25%より速く~約6,000%より速く、約25%より速く~約5,000%より速く、約25%より速く~約4,000%より速く、約25%より速く~約3,000%より速く、約25%より速く~約2,000%より速く、約25%より速く~約1,000%より速く、約25%より速く~約500%より速く、約25%より速く~約480%より速く、約25%より速く~約460%より速く、約25%より速く~約440%より速く、約25%より速く~約420%より速く、約25%より速く~約400%より速く、約25%より速く~約380%より速く、約25%より速く~約360%より速く、約25%より速く~約340%より速く、約25%より速く~約320%より速く、約25%より速く~約300%より速く、約25%より速く~約280%より速く、約25%より速く~約260%より速く、約25%より速く~約240%より速く、約25%より速く~約220%より速く、約25%より速く~約200%より速く、約25%より速く~約180%より速く、約25%より速く~約160%より速く、約25%より速く~約140%より速く、約25%より速く~約120%より速く、約25%より速く~約100%より速く、約25%より速く~約95%より速く、約25%より速く~約90%より速く、約25%より速く~約85%より速く、約25%より速く~約80%より速く、約25%より速く~約75%より速く、約25%より速く~約70%より速く、約25%より速く~約65%より速く、約25%より速く~約60%より速く、約25%より速く~約55%より速く、約25%より速く~約50%より速く、約25%より速く~約45%より速く、約25%より速く~約40%より速く、約25%より速く~約35%より速く、約25%より速く~約30%より速く、約30%より速く~約10,000%より速く、約30%より速く~約9,000%より速く、約30%より速く~約8,000%より速く、約30%より速く~約7,000%より速く、約30%より速く~約6,000%より速く、約30%より速く~約5,000%より速く、約30%より速く~約4,000%より速く、約30%より速く~約3,000%より速く、約30%より速く~約2,000%より速く、約30%より速く~約1,000%より速く、約30%より速く~約500%より速く、約30%より速く~約480%より速く、約30%より速く~約460%より速く、約30%より速く~約440%より速く、約30%より速く~約420%より速く、約30%より速く~約400%より速く、約30%より速く~約380%より速く、約30%より速く~約360%より速く、約30%より速く~約340%より速く、約30%より速く~約320%より速く、約30%より速く~約300%より速く、約30%より速く~約280%より速く、約30%より速く~約260%より速く、約30%より速く~約240%より速く、約30%より速く~約220%より速く、約30%より速く~約200%より速く、約30%より速く~約180%より速く、約30%より速く~約160%より速く、約30%より速く~約140%より速く、約30%より速く~約120%より速く、約30%より速く~約100%より速く、約30%より速く~約95%より速く、約30%より速く~約90%より速く、約30%より速く~約85%より速く、約30%より速く~約80%より速く、約30%より速く~約75%より速く、約30%より速く~約70%より速く、約30%より速く~約65%より速く、約30%より速く~約60%より速く、約30%より速く~約55%より速く、約30%より速く~約50%より速く、約30%より速く~約45%より速く、約30%より速く~約40%より速く、約30%より速く~約35%より速く、約35%より速く~約10,000%より速く、約35%より速く~約9,000%より速く、約35%より速く~約8,000%より速く、約35%より速く~約7,000%より速く、約35%より速く~約6,000%より速く、約35%より速く~約5,000%より速く、約35%より速く~約4,000%より速く、約35%より速く~約3,000%より速く、約35%より速く~約2,000%より速く、約35%より速く~約1,000%より速く、約35%より速く~約500%より速く、約35%より速く~約480%より速く、約35%より速く~約460%より速く、約35%より速く~約440%より速く、約35%より速く~約420%より速く、約35%より速く~約400%より速く、
約35%より速く~約380%より速く、約35%より速く~約360%より速く、約35%より速く~約340%より速く、約35%より速く~約320%より速く、約35%より速く~約300%より速く、約35%より速く~約280%より速く、約35%より速く~約260%より速く、約35%より速く~約240%より速く、約35%より速く~約220%より速く、約35%より速く~約200%より速く、約35%より速く~約180%より速く、約35%より速く~約160%より速く、約35%より速く~約140%より速く、約35%より速く~約120%より速く、約35%より速く~約100%より速く、約35%より速く~約95%より速く、約35%より速く~約90%より速く、約35%より速く~約85%より速く、約35%より速く~約80%より速く、約35%より速く~約75%より速く、約35%より速く~約70%より速く、約35%より速く~約65%より速く、約35%より速く~約60%より速く、約35%より速く~約55%より速く、約35%より速く~約50%より速く、約35%より速く~約45%より速く、約35%より速く~約40%より速く、約40%より速く~約10,000%より速く、約40%より速く~約9,000%より速く、約40%より速く~約8,000%より速く、約40%より速く~約7,000%より速く、約40%より速く~約6,000%より速く、約40%より速く~約5,000%より速く、約40%より速く~約4,000%より速く、約40%より速く~約3,000%より速く、約40%より速く~約2,000%より速く、約40%より速く~約1,000%より速く、約40%より速く~約500%より速く、約40%より速く~約480%より速く、約40%より速く~約460%より速く、約40%より速く~約440%より速く、約40%より速く~約420%より速く、約40%より速く~約400%より速く、約40%より速く~約380%より速く、約40%より速く~約360%より速く、約40%より速く~約340%より速く、約40%より速く~約320%より速く、約40%より速く~約300%より速く、約40%より速く~約280%より速く、約40%より速く~約260%より速く、約40%より速く~約240%より速く、約40%より速く~約220%より速く、約40%より速く~約200%より速く、約40%より速く~約180%より速く、約40%より速く~約160%より速く、約40%より速く~約140%より速く、約40%より速く~約120%より速く、約40%より速く~約100%より速く、約40%より速く~約95%より速く、約40%より速く~約90%より速く、約40%より速く~約85%より速く、約40%より速く~約80%より速く、約40%より速く~約75%より速く、約40%より速く~約70%より速く、約40%より速く~約65%より速く、約40%より速く~約60%より速く、約40%より速く~約55%より速く、約40%より速く~約50%より速く、約40%より速く~約45%より速く、約45%より速く~約10,000%より速く、約45%より速く~約9,000%より速く、約45%より速く~約8,000%より速く、約45%より速く~約7,000%より速く、約45%より速く~約6,000%より速く、約45%より速く~約5,000%より速く、約45%より速く~約4,000%より速く、約45%より速く~約3,000%より速く、約45%より速く~約2,000%より速く、約45%より速く~約1,000%より速く、約45%より速く~約500%より速く、約45%より速く~約480%より速く、約45%より速く~約460%より速く、約45%より速く~約440%より速く、約45%より速く~約420%より速く、約45%より速く~約400%より速く、約45%より速く~約380%より速く、約45%より速く~約360%より速く、約45%より速く~約340%より速く、約45%より速く~約320%より速く、約45%より速く~約300%より速く、約45%より速く~約280%より速く、約45%より速く~約260%より速く、約45%より速く~約240%より速く、約45%より速く~約220%より速く、約45%より速く~約200%より速く、約45%より速く~約180%より速く、約45%より速く~約160%より速く、約45%より速く~約140%より速く、約45%より速く~約120%より速く、約45%より速く~約100%より速く、約45%より速く~約95%より速く、約45%より速く~約90%より速く、約45%より速く~約85%より速く、約45%より速く~約80%より速く、約45%より速く~約75%より速く、約45%より速く~約70%より速く、約45%より速く~約65%より速く、約45%より速く~約60%より速く、約45%より速く~約55%より速く、約45%より速く~約50%より速く、約50%より速く~約10,000%より速く、約50%より速く~約9,000%より速く、約50%より速く~約8,000%より速く、約50%より速く~約7,000%より速く、約50%より速く~約6,000%より速く、約50%より速く~約5,000%より速く、約50%より速く~約4,000%より速く、約50%より速く~約3,000%より速く、約50%より速く~約2,000%より速く、約50%より速く~約1,000%より速く、約50%より速く~約500%より速く、約50%より速く~約480%より速く、約50%より速く~約460%より速く、約50%より速く~約440%より速く、約50%より速く~約420%より速く、約50%より速く~約400%より速く、約50%より速く~約380%より速く、約50%より速く~約360%より速く、約50%より速く~約340%より速く、約50%より速く~約320%より速く、約50%より速く~約300%より速く、約50%より速く~約280%より速く、約50%より速く~約260%より速く、約50%より速く~約240%より速く、約50%より速く~約220%より速く、約50%より速く~約200%より速く、約50%より速く~約180%より速く、約50%より速く~約160%より速く、約50%より速く~約140%より速く、約50%より速く~約120%より速く、約50%より速く~約100%より速く、約50%より速く~約95%より速く、約50%より速く~約90%より速く、約50%より速く~約85%より速く、約50%より速く~約80%より速く、約50%より速く~約75%より速く、約50%より速く~約70%より速く、約50%より速く~約65%より速く、約50%より速く~約60%より速く、約50%より速く~約55%より速く、約55%より速く~約10,000%より速く、約55%より速く~約9,000%より速く、約55%より速く~約8,000%より速く、約55%より速く~約7,000%より速く、約55%より速く~約6,000%より速く、約55%より速く~約5,000%より速く、約55%より速く~約4,000%より速く、約55%より速く~約3,000%より速く、約55%より速く~約2,000%より速く、約55%より速く~約1,000%より速く、約55%より速く~約500%より速く、約55%より速く~約480%より速く、約55%より速く~約460%より速く、約55%より速く~約440%より速く、約55%より速く~約420%より速く、約55%より速く~約400%より速く、約55%より速く~約380%より速く、約55%より速く~約360%より速く、約55%より速く~約340%より速く、約55%より速く~約320%より速く、約55%より速く~約300%より速く、約55%より速く~約280%より速く、約55%より速く~約260%より速く、約55%より速く~約240%より速く、約55%より速く~約220%より速く、約55%より速く~約200%より速く、約55%より速く~約180%より速く、約55%より速く~約160%より速く、約55%より速く~約140%より速く、約55%より速く~約120%より速く、約55%より速く~約100%より速く、約55%より速く~約95%より速く、約55%より速く~約90%より速く、約55%より速く~約85%より速く、約55%より速く~約80%より速く、約55%より速く~約75%より速く、約55%より速く~約70%より速く、約55%より速く~約65%より速く、約55%より速く~約60%より速く、約60%より速く~約10,000%より速く、約60%より速く~約9,000%より速く、約60%より速く~約8,000%より速く、約60%より速く~約7,000%より速く、約60%より速く~約6,000%より速く、約60%より速く~約5,000%より速く、約60%より速く~約4,000%より速く、約60%より速く~約3,000%より速く、約60%より速く~約2,000%より速く、約60%より速く~約1,000%より速く、約60%より速く~約500%より速く、約60%より速く~約480%より速く、約60%より速く~約460%より速く、約60%より速く~約440%より速く、約60%より速く~約420%より速く、約60%より速く~約400%より速く、約60%より速く~約380%より速く、約60%より速く~約360%より速く、約60%より速く~約340%より速く、約60%より速く~約320%より速く、約60%より速く~約300%より速く、約60%より速く~約280%より速く、約60%より速く~約260%より速く、約60%より速く~約240%より速く、約60%より速く~約220%より速く、約60%より速く~約200%より速く、約60%より速く~約180%より速く、約60%より速く~約160%より速く、約60%より速く~約140%より速く、約60%より速く~約120%より速く、約60%より速く~約100%より速く、約60%より速く~約95%より速く、約60%より速く~約90%より速く、約60%より速く~約85%より速く、約60%より速く~約80%より速く、約60%より速く~約75%より速く、約60%より速く~約70%より速く、約60%より速く~約65%より速く、約65%より速く~約10,000%より速く、約65%より速く~約9,000%より速く、約65%より速く~約8,000%より速く、約65%より速く~約7,000%より速く、約65%より速く~約6,000%より速く、約65%より速く~約5,000%より速く、約65%より速く~約4,000%より速く、約65%より速く~約3,000%より速く、約65%より速く~約2,000%より速く、約65%より速く~約1,000%より速く、約65%より速く~約500%より速く、約65%より速く~約480%より速く、約65%より速く~約460%より速く、約65%より速く~約440%より速く、約65%より速く~約420%より速く、約65%より速く~約400%より速く、約65%より速く~約380%より速く、約65%より速く~約360%より速く、約65%より速く~約340%より速く、約65%より速く~約320%より速く、約65%より速く~約300%より速く、約65%より速く~約280%より速く、約65%より速く~約260%より速く、約65%より速く~約240%より速く、約65%より速く~約220%より速く、約65%より速く~約200%より速く、約65%より速く~約180%より速く、約65%より速く~約160%より速く、約65%より速く~約140%より速く、約65%より速く~約120%より速く、約65%より速く~約100%より速く、約65%より速く~約95%より速く、約65%より速く~約90%より速く、約65%より速く~約85%より速く、約65%より速く~約80%より速く、約65%より速く~約75%より速く、約65%より速く~約70%より速く、約70%より速く~約10,000%より速く、約70%より速く~約9,000%より速く
、約70%より速く~約8,000%より速く、約70%より速く~約7,000%より速く、約70%より速く~約6,000%より速く、約70%より速く~約5,000%より速く、約70%より速く~約4,000%より速く、約70%より速く~約3,000%より速く、約70%より速く~約2,000%より速く、約70%より速く~約1,000%より速く、約70%より速く~約500%より速く、約70%より速く~約480%より速く、約70%より速く~約460%より速く、約70%より速く~約440%より速く、約70%より速く~約420%より速く、約70%より速く~約400%より速く、約70%より速く~約380%より速く、約70%より速く~約360%より速く、約70%より速く~約340%より速く、約70%より速く~約320%より速く、約70%より速く~約300%より速く、約70%より速く~約280%より速く、約70%より速く~約260%より速く、約70%より速く~約240%より速く、約70%より速く~約220%より速く、約70%より速く~約200%より速く、約70%より速く~約180%より速く、約70%より速く~約160%より速く、約70%より速く~約140%より速く、約70%より速く~約120%より速く、約70%より速く~約100%より速く、約70%より速く~約95%より速く、約70%より速く~約90%より速く、約70%より速く~約85%より速く、約70%より速く~約80%より速く、約70%より速く~約75%より速く、約75%より速く~約10,000%より速く、約75%より速く~約9,000%より速く、約75%より速く~約8,000%より速く、約75%より速く~約7,000%より速く、約75%より速く~約6,000%より速く、約75%より速く~約5,000%より速く、約75%より速く~約4,000%より速く、約75%より速く~約3,000%より速く、約75%より速く~約2,000%より速く、約75%より速く~約1,000%より速く、約75%より速く~約500%より速く、約75%より速く~約480%より速く、約75%より速く~約460%より速く、約75%より速く~約440%より速く、約75%より速く~約420%より速く、約75%より速く~約400%より速く、約75%より速く~約380%より速く、約75%より速く~約360%より速く、約75%より速く~約340%より速く、約75%より速く~約320%より速く、約75%より速く~約300%より速く、約75%より速く~約280%より速く、約75%より速く~約260%より速く、約75%より速く~約240%より速く、約75%より速く~約220%より速く、約75%より速く~約200%より速く、約75%より速く~約180%より速く、約75%より速く~約160%より速く、約75%より速く~約140%より速く、約75%より速く~約120%より速く、約75%より速く~約100%より速く、約75%より速く~約95%より速く、約75%より速く~約90%より速く、約75%より速く~約85%より速く、約75%より速く~約80%より速く、約80%より速く~約10,000%より速く、約80%より速く~約9,000%より速く、約80%より速く~約8,000%より速く、約80%より速く~約7,000%より速く、約80%より速く~約6,000%より速く、約80%より速く~約5,000%より速く、約80%より速く~約4,000%より速く、約80%より速く~約3,000%より速く、約80%より速く~約2,000%より速く、約80%より速く~約1,000%より速く、約80%より速く~約500%より速く、約80%より速く~約480%より速く、約80%より速く~約460%より速く、約80%より速く~約440%より速く、約80%より速く~約420%より速く、約80%より速く~約400%より速く、約80%より速く~約380%より速く、約80%より速く~約360%より速く、約80%より速く~約340%より速く、約80%より速く~約320%より速く、約80%より速く~約300%より速く、約80%より速く~約280%より速く、約80%より速く~約260%より速く、約80%より速く~約240%より速く、約80%より速く~約220%より速く、約80%より速く~約200%より速く、約80%より速く~約180%より速く、約80%より速く~約160%より速く、約80%より速く~約140%より速く、約80%より速く~約120%より速く、約80%より速く~約100%より速く、約80%より速く~約95%より速く、約80%より速く~約90%より速く、約80%より速く~約85%より速く、約85%より速く~約10,000%より速く、約85%より速く~約9,000%より速く、約85%より速く~約8,000%より速く、約85%より速く~約7,000%より速く、約85%より速く~約6,000%より速く、約85%より速く~約5,000%より速く、約85%より速く~約4,000%より速く、約85%より速く~約3,000%より速く、約85%より速く~約2,000%より速く、約85%より速く~約1,000%より速く、約85%より速く~約500%より速く、約85%より速く~約480%より速く、約85%より速く~約460%より速く、約85%より速く~約440%より速く、約85%より速く~約420%より速く、約85%より速く~約400%より速く、約85%より速く~約380%より速く、約85%より速く~約360%より速く、約85%より速く~約340%より速く、約85%より速く~約320%より速く、約85%より速く~約300%より速く、約85%より速く~約280%より速く、約85%より速く~約260%より速く、約85%より速く~約240%より速く、約85%より速く~約220%より速く、約85%より速く~約200%より速く、約85%より速く~約180%より速く、約85%より速く~約160%より速く、約85%より速く~約140%より速く、約85%より速く~約120%より速く、約85%より速く~約100%より速く、約85%より速く~約95%より速く、約85%より速く~約90%より速く、約90%より速く~約10,000%より速く、約90%より速く~約9,000%より速く、約90%より速く~約8,000%より速く、約90%より速く~約7,000%より速く、約90%より速く~約6,000%より速く、約90%より速く~約5,000%より速く、約90%より速く~約4,000%より速く、約90%より速く~約3,000%より速く、約90%より速く~約2,000%より速く、約90%より速く~約1,000%より速く、約90%より速く~約500%より速く、約90%より速く~約480%より速く、約90%より速く~約460%より速く、約90%より速く~約440%より速く、約90%より速く~約420%より速く、約90%より速く~約400%より速く、約90%より速く~約380%より速く、約90%より速く~約360%より速く、約90%より速く~約340%より速く、約90%より速く~約320%より速く、約90%より速く~約300%より速く、約90%より速く~約280%より速く、約90%より速く~約260%より速く、約90%より速く~約240%より速く、約90%より速く~約220%より速く、約90%より速く~約200%より速く、約90%より速く~約180%より速く、約90%より速く~約160%より速く、約90%より速く~約140%より速く、約90%より速く~約120%より速く、約90%より速く~約100%より速く、約90%より速く~約95%より速く、約95%より速く~約10,000%より速く、約95%より速く~約9,000%より速く、約95%より速く~約8,000%より速く、約95%より速く~約7,000%より速く、約95%より速く~約6,000%より速く、約95%より速く~約5,000%より速く、約95%より速く~約4,000%より速く、約95%より速く~約3,000%より速く、約95%より速く~約2,000%より速く、約95%より速く~約1,000%より速く、約95%より速く~約500%より速く、約95%より速く~約480%より速く、約95%より速く~約460%より速く、約95%より速く~約440%より速く、約95%より速く~約420%より速く、約95%より速く~約400%より速く、約95%より速く~約380%より速く、約95%より速く~約360%より速く、約95%より速く~約340%より速く、約95%より速く~約320%より速く、約95%より速く~約300%より速く、約95%より速く~約280%より速く、約95%より速く~約260%より速く、約95%より速く~約240%より速く、約95%より速く~約220%より速く、約95%より速く~約200%より速く、約95%より速く~約180%より速く、約95%より速く~約160%より速く、約95%より速く~約140%より速く、約95%より速く~約120%より速く、約95%より速く~約100%より速く、約100%より速く~約10,000%より速く、約100%より速く~約9,000%より速く、約100%より速く~約8,000%より速く、約100%より速く~約7,000%より速く、約100%より速く~約6,000%より速く、約100%より速く~約5,000%より速く、約100%より速く~約4,000%より速く、約100%より速く~約3,000%より速く、約100%より速く~約2,000%より速く、約100%より速く~約1,000%より速く、約100%より速く~約500%より速く、約100%より速く~約480%より速く、約100%より速く~約460%より速く、約100%より速く~約440%より速く、約100%より速く~約420%より速く、約100%より速く~約400%より速く、約100%より速く~約380%より速く、約100%より速く~約360%より速く、約100%より速く~約340%より速く、約100%より速く~約320%より速く、約100%より速く~約300%より速く、約100%より速く~約280%より速く、約100%より速く~約260%より速く、約100%より速く~約240%より速く、約100%より速く~約220%より速く、約100%より速く~約200%より速く、約100%より速く~約180%より速く、約100%より速く~約160%より速く、約100%より速く~約140%より速く、約100%より速く~約120%より速く、約120%より速く~約10,000%より速く、約120%より速く~約9,000%より速く、約120%より速く~約8,000%より速く、約120%より速く~約7,000%より速く、約120%より速く~約6,000%より速く、約120%より速く~約5000%より速く、約120%より速く~約4,000%より速く、約120%より速く~約3,000%より速く、約120%より速く~約2,000%より速く、約120%より速く~約1,000%より速く、約120%より速く~約500%より速く、約120%より速く~約480%より速く、約120%より速く~約460%より速く、約120%より速く~約440%より速く、約120%より速く~約420%より速く、約120%より速く~約400%より速く、約120%より速く~約380%より速く、約120%より速く~約360%より速く、約120%より速く~約340%より速く、約120%より速く~約320%より速く、約120%より速く~約300%より速く、約120%より速く~約280%より速く、約120%より速く~約260%より速く、約120%より速く~約240%より速く、約120%より速く~約220%より速く、約120%より速く~約200%より速く、約120%より速く~約180%より速く、約120%より速く~約160%より速く、約120%より速く~約140%より速く、約140%より速く~約1
0,000%より速く、約140%より速く~約9,000%より速く、約140%より速く~約8,000%より速く、約140%より速く~約7,000%より速く、約140%より速く~約6,000%より速く、約140%より速く~約5,000%より速く、約140%より速く~約4,000%より速く、約140%より速く~約3,000%より速く、約140%より速く~約2,000%より速く、約140%より速く~約1,000%より速く、約140%より速く~約500%より速く、約140%より速く~480%より速く、約140%より速く~約460%より速く、約140%より速く~約440%より速く、約140%より速く~約420%より速く、約140%より速く~約400%より速く、約140%より速く~約380%より速く、約140%より速く~約360%より速く、約140%より速く~約340%より速く、約140%より速く~約320%より速く、約140%より速く~約300%より速く、約140%より速く~約280%より速く、約140%より速く~約260%より速く、約140%より速く~約240%より速く、約140%より速く~約220%より速く、約140%より速く~約200%より速く、約140%より速く~約180%より速く、約140%より速く~約160%より速く、約160%より速く~約10,000%より速く、約160%より速く~約9,000%より速く、約160%より速く~約8,000%より速く、約160%より速く~約7,000%より速く、約160%より速く~約6,000%より速く、約160%より速く~約5,000%より速く、約160%より速く~約4,000%より速く、約160%より速く~約3,000%より速く、約160%より速く~約2,000%より速く、約160%より速く~約1,000%より速く、約160%より速く~約500%より速く、約160%より速く~約480%より速く、約160%より速く~約460%より速く、約160%より速く~約440%より速く、約160%より速く~約420%より速く、約160%より速く~約400%より速く、約160%より速く~約380%より速く、約160%より速く~約360%より速く、約160%より速く~約340%より速く、約160%より速く~約320%より速く、約160%より速く~約300%より速く、約160%より速く~約280%より速く、約160%より速く~約260%より速く、約160%より速く~約240%より速く、約160%より速く~約220%より速く、約160%より速く~約200%より速く、約160%より速く~約180%より速く、約180%より速く~約10,000%より速く、約180%より速く~約9,000%より速く、約180%より速く~約8,000%より速く、約180%より速く~約7,000%より速く、約180%より速く~約6,000%より速く、約180%より速く~約5,000%より速く、約180%より速く~約4,000%より速く、約180%より速く~約3,000%より速く、約180%より速く~約2,000%より速く、約180%より速く~約1,000%より速く、約180%より速く~約500%より速く、約180%より速く~約480%より速く、約180%より速く~約460%より速く、約180%より速く~約440%より速く、約180%より速く~約420%より速く、約180%より速く~約400%より速く、約180%より速く~約380%より速く、約180%より速く~約360%より速く、約180%より速く~約340%より速く、約180%より速く~約320%より速く、約180%より速く~約300%より速く、約180%より速く~約280%より速く、約180%より速く~約260%より速く、約180%より速く~約240%より速く、約180%より速く~約220%より速く、約180%より速く~約200%より速く、約200%より速く~約10,000%より速く、約200%より速く~約9,000%より速く、約200%より速く~約8,000%より速く、約200%より速く~約7,000%より速く、約200%より速く~約6,000%より速く、約200%より速く~約5,000%より速く、約200%より速く~約4,000%より速く、約200%より速く~約3,000%より速く、約200%より速く~約2,000%より速く、約200%より速く~約1,000%より速く、約200%より速く~約500%より速く、約200%より速く~約480%より速く、約200%より速く~約460%より速く、約200%より速く~約440%より速く、約200%より速く~約420%より速く、約200%より速く~約400%より速く、約200%より速く~約380%より速く、約200%より速く~約360%より速く、約200%より速く~約340%より速く、約200%より速く~約320%より速く、約200%より速く~約300%より速く、約200%より速く~約280%より速く、約200%より速く~約260%より速く、約200%より速く~約240%より速く、約200%より速く~約220%より速く、約220%より速く~約10,000%より速く、約220%より速く~約9,000%より速く、約220%より速く~約8,000%より速く、約220%より速く~約7,000%より速く、約220%より速く~約6,000%より速く、約220%より速く~約5,000%より速く、約220%より速く~約4,000%より速く、約220%より速く~約3,000%より速く、約220%より速く~約2,000%より速く、約220%より速く~約1,000%より速く、約220%より速く~約500%より速く、約220%より速く~約480%より速く、約220%より速く~約460%より速く、約220%より速く~約440%より速く、約220%より速く~約420%より速く、約220%より速く~約400%より速く、約220%より速く~約380%より速く、約220%より速く~約360%より速く、約220%より速く~約340%より速く、約220%より速く~約320%より速く、約220%より速く~約300%より速く、約220%より速く~約280%より速く、約220%より速く~約260%より速く、約220%より速く~約240%より速く、約240%より速く~約10,000%より速く、約240%より速く~約9,000%より速く、約240%より速く~約8,000%より速く、約240%より速く~約7,000%より速く、約240%より速く~約6,000%より速く、約240%より速く~約5,000%より速く、約240%より速く~約4,000%より速く、約240%より速く~約3,000%より速く、約240%より速く~約2,000%より速く、約240%より速く~約1,000%より速く、約240%より速く~約500%より速く、約240%より速く~約480%より速く、約240%より速く~約460%より速く、約240%より速く~約440%より速く、約240%より速く~約420%より速く、約240%より速く~約400%より速く、約240%より速く~約380%より速く、約240%より速く~約360%より速く、約240%より速く~約340%より速く、約240%より速く~約320%より速く、約240%より速く~約300%より速く、約240%より速く~約280%より速く、約240%より速く~約260%より速く、約260%より速く~約10,000%より速く、約260%より速く~約9,000%より速く、約260%より速く~約8,000%より速く、約260%より速く~約7,000%より速く、約260%より速く~約6,000%より速く、約260%より速く~約5,000%より速く、約260%より速く~約4,000%より速く、約260%より速く~約3,000%より速く、約260%より速く~約2,000%より速く、約260%より速く~約1,000%より速く、約260%より速く~約500%より速く、約260%より速く~約480%より速く、約260%より速く~約460%より速く、約260%より速く~約440%より速く、約260%より速く~約420%より速く、約260%より速く~約400%より速く、約260%より速く~約380%より速く、約260%より速く~約360%より速く、約260%より速く~約340%より速く、約260%より速く~約320%より速く、約260%より速く~約300%より速く、約260%より速く~約280%より速く、約280%より速く~約10,000%より速く、約280%より速く~約9,000%より速く、約280%より速く~約8,000%より速く、約280%より速く~約7,000%より速く、約280%より速く~約6,000%より速く、約280%より速く~約5,000%より速く、約280%より速く~約4,000%より速く、約280%より速く~約3,000%より速く、約280%より速く~約2,000%より速く、約280%より速く~約1,000%より速く、約280%より速く~約500%より速く、約280%より速く~約480%より速く、約280%より速く~約460%より速く、約280%より速く~約440%より速く、約280%より速く~約420%より速く、約280%より速く~約400%より速く、約280%より速く~約380%より速く、約280%より速く~約360%より速く、約280%より速く~約340%より速く、約280%より速く~約320%より速く、約280%より速く~約300%より速く、約300%より速く~約10,000%より速く、約300%より速く~約9,000%より速く、約300%より速く~約8,000%より速く、約300%より速く~約7,000%より速く、約300%より速く~約6,000%より速く、約300%より速く~約5,000%より速く、約300%より速く~約4,000%より速く、約300%より速く~約3,000%より速く、約300%より速く~約2,000%より速く、約300%より速く~約1,000%より速く、約300%より速く~約500%より速く、約300%より速く~約480%より速く、約300%より速く~約460%より速く、約300%より速く~約440%より速く、約300%より速く~約420%より速く、約300%より速く~約400%より速く、約300%より速く~約380%より速く、約300%より速く~約360%より速く、約300%より速く~約340%より速く、約300%より速く~約320%より速く、約320%より速く~約10,000%より速く、約320%より速く~約9,000%より速く、約320%より速く~約8,000%より速く、約320%より速く~約7,000%より速く、約320%より速く~約6,000%より速く、約320%より速く~約5,000%より速く、約320%より速く~約4,000%より速く、約320%より速く~約3,000%より速く、約320%より速く~約2,000%より速く、約320%より速く~約1,000%より速く、約320%より速く~約500%より速く、約320%より速く~約480%より速く、約320%より速く~約460%より速く、約320%より速く~約440%より速く、約320%より速く~約420%より速く、約320%より速く~約400%より速く、約320%より速く~約380%より速く、約320%より速く~約360%より速く、約320%より速く~約340%より速く、約340%より速く~約10,000%より速く、約340%より速く~約9,000%より速く、約340%より速く~約8,000%より速く、約340%より速く~約7,000%より速く、約340%より速く~約6,000%より速く、約340%より速く~約5,000%より速く、約340%より速く~約4,000%より速く、約340%より速く~約3,000%より速く、約340%より速く~約2,000%より速く、約340%より速く~約1,000%より速く、約34
0%より速く~約500%より速く、約340%より速く~約480%より速く、約340%より速く~約460%より速く、約340%より速く~約440%より速く、約340%より速く~約420%より速く、約340%より速く~約400%より速く、約340%より速く~約380%より速く、約340%より速く~約360%より速く、約360%より速く~約10,000%より速く、約360%より速く~約9,000%より速く、約360%より速く~約8,000%より速く、約360%より速く~約7,000%より速く、約360%より速く~約6,000%より速く、約360%より速く~約5,000%より速く、約360%より速く~約4,000%より速く、約360%より速く~約3,000%より速く、約360%より速く~約2,000%より速く、約360%より速く~約1,000%より速く、約360%より速く~約500%より速く、約360%より速く~約480%より速く、約360%より速く~約460%より速く、約360%より速く~約440%より速く、約360%より速く~約420%より速く、約360%より速く~約400%より速く、約360%より速く~約380%より速く、約380%より速く~約10,000%より速く、約380%より速く~約9,000%より速く、約380%より速く~約8,000%より速く、約380%より速く~約7,000%より速く、約380%より速く~約6,000%より速く、約380%より速く~約5,000%より速く、約380%より速く~約4,000%より速く、約380%より速く~約3,000%より速く、約380%より速く~約2,000%より速く、約380%より速く~約1,000%より速く、約380%より速く~約500%より速く、約380%より速く~約480%より速く、約380%より速く~約460%より速く、約380%より速く~約440%より速く、約380%より速く~約420%より速く、約380%より速く~約400%より速く、約400%より速く~約10,000%より速く、約400%より速く~約9,000%より速く、約400%より速く~約8,000%より速く、約400%より速く~約7,000%より速く、約400%より速く~約6,000%より速く、約400%より速く~約5,000%より速く、約400%より速く~約4,000%より速く、約400%より速く~約3,000%より速く、約400%より速く~約2,000%より速く、約400%より速く~約1,000%より速く、約400%より速く~約500%より速く、約400%より速く~約480%より速く、約400%より速く~約460%より速く、約400%より速く~約440%より速く、約400%より速く~約420%より速く、約420%より速く~約10,000%より速く、約420%より速く~約9,000%より速く、約420%より速く~約8,000%より速く、約420%より速く~約7,000%より速く、約420%より速く~約6,000%より速く、約420%より速く~約5,000%より速く、約420%より速く~約4,000%より速く、約420%より速く~約3,000%より速く、約420%より速く~約2,000%より速く、約420%より速く~約1,000%より速く、約420%より速く~約500%より速く、約420%より速く~約480%より速く、約420%より速く~約460%より速く、約420%より速く~約440%より速く、約440%より速く~約10,000%より速く、約440%より速く~約9,000%より速く、約440%より速く~約8,000%より速く、約440%より速く~約7,000%より速く、約440%より速く~約6,000%より速く、約440%より速く~約5,000%より速く、約440%より速く~約4,000%より速く、約440%より速く~約3,000%より速く、約440%より速く~約2,000%より速く、約440%より速く~約1,000%より速く、約440%より速く~約500%より速く、約440%より速く~約480%より速く、約440%より速く~約460%より速く、約460%より速く~約10,000%より速く、約460%より速く~約9,000%より速く、約460%より速く~約8,000%より速く、約460%より速く~約7,000%より速く、約460%より速く~約6,000%より速く、約460%より速く~約5,000%より速く、約460%より速く~約4,000%より速く、約460%より速く~約3,000%より速く、約460%より速く~約2,000%より速く、約460%より速く~約1,000%より速く、約460%より速く~約500%より速く、約460%より速く~約480%より速く、約480%より速く~約10,000%より速く、約480%より速く~約9,000%より速く、約480%より速く~約8,000%より速く、約480%より速く~約7,000%より速く、約480%より速く~約6,000%より速く、約480%より速く~約5,000%より速く、約480%より速く~約4,000%より速く、約480%より速く~約3,000%より速く、約480%より速く~約2,000%より速く、約480%より速く~約1,000%より速く、約480%より速く~約500%より速く、約500%より速く~約10,000%より速く、約500%より速く~約9,000%より速く、約500%より速く~約8,000%より速く、約500%より速く~約7,000%より速く、約500%より速く~約6,000%より速く、約500%より速く~約5,000%より速く、約500%より速く~約4,000%より速く、約500%より速く~約3,000%より速く、約500%より速く~約2,000%より速く、約500%より速く~約1,000%より速く、約1,000%より速く~約10,000%より速く、約1,000%より速く~約9,000%より速く、約1,000%より速く~約8,000%より速く、約1,000%より速く~約7,000%より速く、約1,000%より速く~約6,000%より速く、約1,000%より速く~約5,000%より速く、約1,000%より速く~約4,000%より速く、約1,000%より速く~約3,000%より速く、約1,000%より速く~約2,000%より速く、約2,000%より速く~約10,000%より速く、約2,000%より速く~約9,000%より速く、約2,000%より速く~約8,000%より速く、約2,000%より速く~約7,000%より速く、約2,000%より速く~約6,000%より速く、約2,000%より速く~約5,000%より速く、約2,000%より速く~約4,000%より速く、約2,000%より速く~約3,000%より速く、約3,000%より速く~約10,000%より速く、約3,000%より速く~約9,000%より速く、約3,000%より速く~約8,000%より速く、約3,000%より速く~約7,000%より速く、約3,000%より速く~約6,000%より速く、約3,000%より速く~約5,000%より速く、約3,000%より速く~約4,000%より速く、約4,000%より速く~約10,000%より速く、約4,000%より速く~約9,000%より速く、約4,000%より速く~約8,000%より速く、約4,000%より速く~約7,000%より速く、約4,000%より速く~約6,000%より速く、約4,000%より速く~約5,000%より速く、約5,000%より速く~約10,000%より速く、約5,000%より速く~約9,000%より速く、約5,000%より速く~約8,000%より速く、約5,000%より速く~約7,000%より速く、約5,000%より速く~約6,000%より速く、約6,000%より速く~約10,000%より速く、約6,000%より速く~約9,000%より速く、約6,000%より速く~約8,000%より速く、約6,000%より速く~約7,000%より速く、約7,000%より速く~約10,000%より速く、約7,000%より速く~約9,000%より速く、約7,000%より速く~約8,000%より速く、約8,000%より速く~約10,000%より速く、約8,000%より速く~約9,000%より速く、または約9,000%より速く~約10,000%より速く)。
0%大きい、約30%大きい~約380%大きい、約30%大きい~約360%大きい、約30%大きい~約340%大きい、約30%大きい~約320%大きい、約30%大きい~約300%大きい、約30%大きい~約280%大きい、約30%大きい~約260%大きい、約30%大きい~約240%大きい、約30%大きい~約220%大きい、約30%大きい~約200%大きい、約30%大きい~約180%大きい、約30%大きい~約160%大きい、約30%大きい~約140%大きい、約30%大きい~約120%大きい、約30%大きい~約100%大きい、約30%大きい~約95%大きい、約30%大きい~約90%大きい、約30%大きい~約85%大きい、約30%大きい~約80%大きい、約30%大きい~約75%大きい、約30%大きい~約70%大きい、約30%大きい~約65%大きい、約30%大きい~約60%大きい、約30%大きい~約55%大きい、約30%大きい~約50%大きい、約30%大きい~約45%大きい、約30%大きい~約40%大きい、約30%大きい~約35%大きい、約35%大きい~約10,000%大きい、約35%大きい~約9,000%大きい、約35%大きい~約8,000%大きい、約35%大きい~約7,000%大きい、約35%大きい~約6,000%大きい、約35%大きい~約5,000%大きい、約35%大きい~約4,000%大きい、約35%大きい~約3,000%大きい、約35%大きい~約2,000%大きい、約35%大きい~約1,000%大きい、約35%大きい~約500%大きい、約35%大きい~約480%大きい、約35%大きい~約460%大きい、約35%大きい~約440%大きい、約35%大きい~約420%大きい、約35%大きい~約400%大きい、約35%大きい~約380%大きい、約35%大きい~約360%大きい、約35%大きい~約340%大きい、約35%大きい~約320%大きい、約35%大きい~約300%大きい、約35%大きい~約280%大きい、約35%大きい~約260%大きい、約35%大きい~約240%大きい、約35%大きい~約220%大きい、約35%大きい~約200%大きい、約35%大きい~約180%大きい、約35%大きい~約160%大きい、約35%大きい~約140%大きい、約35%大きい~約120%大きい、約35%大きい~約100%大きい、約35%大きい~約95%大きい、約35%大きい~約90%大きい、約35%大きい~約85%大きい、約35%大きい~約80%大きい、約35%大きい~約75%大きい、約35%大きい~約70%大きい、約35%大きい~約65%大きい、約35%大きい~約60%大きい、約35%大きい~約55%大きい、約35%大きい~約50%大きい、約35%大きい~約45%大きい、約35%大きい~約40%大きい、約40%大きい~約10,000%大きい、約40%大きい~約9,000%大きい、約40%大きい~約8,000%大きい、約40%大きい~約7,000%大きい、約40%大きい~約6,000%大きい、約40%大きい~約5,000%大きい、約40%大きい~約4,000%大きい、約40%大きい~約3,000%大きい、約40%大きい~約2,000%大きい、約40%大きい~約1,000%大きい、約40%大きい~約500%大きい、約40%大きい~約480%大きい、約40%大きい~約460%大きい、約40%大きい~約440%大きい、約40%大きい~約420%大きい、約40%大きい~約400%大きい、約40%大きい~約380%大きい、約40%大きい~約360%大きい、約40%大きい~約340%大きい、約40%大きい~約320%大きい、約40%大きい~約300%大きい、約40%大きい~約280%大きい、約40%大きい~約260%大きい、約40%大きい~約240%大きい、約40%大きい~約220%大きい、約40%大きい~約200%大きい、約40%大きい~約180%大きい、約40%大きい~約160%大きい、約40%大きい~約140%大きい、約40%大きい~約120%大きい、約40%大きい~約100%大きい、約40%大きい~約95%大きい、約40%大きい~約90%大きい、約40%大きい~約85%大きい、約40%大きい~約80%大きい、約40%大きい~約75%大きい、約40%大きい~約70%大きい、約40%大きい~約65%大きい、約40%大きい~約60%大きい、約40%大きい~約55%大きい、約40%大きい~約50%大きい、約40%大きい~約45%大きい、約45%大きい~約10,000%大きい、約45%大きい~約9,000%大きい、約45%大きい~約8,000%大きい、約45%大きい~約7,000%大きい、約45%大きい~約6,000%大きい、約45%大きい~約5,000%大きい、約45%大きい~約4,000%大きい、約45%大きい~約3,000%大きい、約45%大きい~約2,000%大きい、約45%大きい~約1,000%大きい、約45%大きい~約500%大きい、約45%大きい~約480%大きい、約45%大きい~約460%大きい、約45%大きい~約440%大きい、約45%大きい~約420%大きい、約45%大きい~約400%大きい、約45%大きい~約380%大きい、約45%大きい~約360%大きい、約45%大きい~約340%大きい、約45%大きい~約320%大きい、約45%大きい~約300%大きい、約45%大きい~約280%大きい、約45%大きい~約260%大きい、約45%大きい~約240%大きい、約45%大きい~約220%大きい、約45%大きい~約200%大きい、約45%大きい~約180%大きい、約45%大きい~約160%大きい、約45%大きい~約140%大きい、約45%大きい~約120%大きい、約45%大きい~約100%大きい、約45%大きい~約95%大きい、約45%大きい~約90%大きい、約45%大きい~約85%大きい、約45%大きい~約80%大きい、約45%大きい~約75%大きい、約45%大きい~約70%大きい、約45%大きい~約65%大きい、約45%大きい~約60%大きい、約45%大きい~約55%大きい、約45%大きい~約50%大きい、約50%大きい~約10,000%大きい、約50%大きい~約9,000%大きい、約50%大きい~約8,000%大きい、約50%大きい~約7,000%大きい、約50%大きい~約6,000%大きい、約50%大きい~約5,000%大きい、約50%大きい~約4,000%大きい、約50%大きい~約3,000%大きい、約50%大きい~約2,000%大きい、約50%大きい~約1,000%大きい、約50%大きい~約500%大きい、約50%大きい~約480%大きい、約50%大きい~約460%大きい、約50%大きい~約440%大きい、約50%大きい~約420%大きい、約50%大きい~約400%大きい、約50%大きい~約380%大きい、約50%大きい~約360%大きい、約50%大きい~約340%大きい、約50%大きい~約320%大きい、約50%大きい~約300%大きい、約50%大きい~約280%大きい、約50%大きい~約260%大きい、約50%大きい~約240%大きい、約50%大きい~約220%大きい、約50%大きい~約200%大きい、約50%大きい~約180%大きい、約50%大きい~約160%大きい、約50%大きい~約140%大きい、約50%大きい~約120%大きい、約50%大きい~約100%大きい、約50%大きい~約95%大きい、約50%大きい~約90%大きい、約50%大きい~約85%大きい、約50%大きい~約80%大きい、約50%大きい~約75%大きい、約50%大きい~約70%大きい、約50%大きい~約65%大きい、約50%大きい~約60%大きい、約50%大きい~約55%大きい、約55%大きい~約10,000%大きい、約55%大きい~約9,000%大きい、約55%大きい~約8,000%大きい、約55%大きい~約7,000%大きい、約55%大きい~約6,000%大きい、約55%大きい~約5,000%大きい、約55%大きい~約4,000%大きい、約55%大きい~約3,000%大きい、約55%大きい~約2,000%大きい、約55%大きい~約1,000%大きい、約55%大きい~約500%大きい、約55%大きい~約480%大きい、約55%大きい~約460%大きい、約55%大きい~約440%大きい、約55%大きい~約420%大きい、約55%大きい~約400%大きい、約55%大きい~約380%大きい、約55%大きい~約360%大きい、約55%大きい~約340%大きい、約55%大きい~約320%大きい、約55%大きい~約300%大きい、約55%大きい~約280%大きい、約55%大きい~約260%大きい、約55%大きい~約240%大きい、約55%大きい~約220%大きい、約55%大きい~約200%大きい、約55%大きい~約180%大きい、約55%大きい~約160%大きい、約55%大きい~約140%大きい、約55%大きい~約120%大きい、約55%大きい~約100%大きい、約55%大きい~約95%大きい、約55%大きい~約90%大きい、約55%大きい~約85%大きい、約55%大きい~約80%大きい、約55%大きい~約75%大きい、約55%大きい~約70%大きい、約55%大きい~約65%大きい、約55%大きい~約60%大きい、約60%大きい~約10,000%大きい、約60%大きい~約9,000%大きい、約60%大きい~約8,000%大きい、約60%大きい~約7,000%大きい、約60%大きい~約6,000%大きい、約60%大きい~約5,000%大きい、約60%大きい~約4,000%大きい、約60%大きい~約3,000%大きい、約60%大きい~約2,000%大きい、約60%大きい~約1,000%大きい、約60%大きい~約500%大きい、約60%大きい~約480%大きい、約60%大きい~約460%大きい、約60%大きい~約440%大きい、約60%大きい~約420%大きい、約60%大きい~約400%大きい、約60%大きい~約380%大きい、約60%大きい~約360%大きい、約60%大きい~約340%大きい、約60%大きい~約320%大きい、約60%大きい~約300%大きい、約60%大きい~約280%大きい、約60%大きい~約260%大きい、約60%大きい~約240%大きい、約60%大きい~約220%大きい、約60%大きい~約200%大きい、約60%大きい~約180%大きい、約60%大きい~約160%大きい、約60%大きい~約140%大きい、約60%大きい~約120%大きい、約60%大きい~約100%大きい、約60%大きい~約95%大きい、約60%大きい~約90%大きい、約60%大きい~約85%大きい、約60%大きい~約80%大きい、約60%大きい~約75%大きい、約60%大きい~約70%大きい、約60%大きい~約65%大きい、約65%大きい~約10,000%大きい、約65%大きい~約9,000%大きい、約65%大きい~約8,000%大きい、約65%大きい~約7,000%大きい、約65%大きい~約6,000%大きい、約65%大きい~約5,000%大きい、約65%大きい~約4,000%大きい、約65%大きい~約3,000%大きい、約65%大きい~約2,000%大きい、約65%大きい~約1,000%大きい、約65%大きい~約500%大きい、約65%大きい~約480%大きい、約65%大きい~約460%大きい、約65%大きい~約440%大きい、約65%大きい~約420%大きい、約65%大きい~約400%大きい、約65%大きい~約380%大きい、約65%大きい~約360%大きい、約65%大きい~約340%大きい、約65%大きい~約320%大きい、約65%大きい~約300%大きい、約65%大きい~約280%大きい、約65%大きい~約260%大きい、約65%大きい~約240%大きい、約65%大きい~約220%大きい、約65%大き
い~約200%大きい、約65%大きい~約180%大きい、約65%大きい~約160%大きい、約65%大きい~約140%大きい、約65%大きい~約120%大きい、約65%大きい~約100%大きい、約65%大きい~約95%大きい、約65%大きい~約90%大きい、約65%大きい~約85%大きい、約65%大きい~約80%大きい、約65%大きい~約75%大きい、約65%大きい~約70%大きい、約70%大きい~約10,000%大きい、約70%大きい~約9,000%大きい、約70%大きい~約8,000%大きい、約70%大きい~約7,000%大きい、約70%大きい~約6,000%大きい、約70%大きい~約5,000%大きい、約70%大きい~約4,000%大きい、約70%大きい~約3,000%大きい、約70%大きい~約2,000%大きい、約70%大きい~約1,000%大きい、約70%大きい~約500%大きい、約70%大きい~約480%大きい、約70%大きい~約460%大きい、約70%大きい~約440%大きい、約70%大きい~約420%大きい、約70%大きい~約400%大きい、約70%大きい~約380%大きい、約70%大きい~約360%大きい、約70%大きい~約340%大きい、約70%大きい~約320%大きい、約70%大きい~約300%大きい、約70%大きい~約280%大きい、約70%大きい~約260%大きい、約70%大きい~約240%大きい、約70%大きい~約220%大きい、約70%大きい~約200%大きい、約70%大きい~約180%大きい、約70%大きい~約160%大きい、約70%大きい~約140%大きい、約70%大きい~約120%大きい、約70%大きい~約100%大きい、約70%大きい~約95%大きい、約70%大きい~約90%大きい、約70%大きい~約85%大きい、約70%大きい~約80%大きい、約70%大きい~約75%大きい、約75%大きい~約10,000%大きい、約75%大きい~約9,000%大きい、約75%大きい~約8,000%大きい、約75%大きい~約7,000%大きい、約75%大きい~約6,000%大きい、約75%大きい~約5,000%大きい、約75%大きい~約4,000%大きい、約75%大きい~約3,000%大きい、約75%大きい~約2,000%大きい、約75%大きい~約1,000%大きい、約75%大きい~約500%大きい、約75%大きい~約480%大きい、約75%大きい~約460%大きい、約75%大きい~約440%大きい、約75%大きい~約420%大きい、約75%大きい~約400%大きい、約75%大きい~約380%大きい、約75%大きい~約360%大きい、約75%大きい~約340%大きい、約75%大きい~約320%大きい、約75%大きい~約300%大きい、約75%大きい~約280%大きい、約75%大きい~約260%大きい、約75%大きい~約240%大きい、約75%大きい~約220%大きい、約75%大きい~約200%大きい、約75%大きい~約180%大きい、約75%大きい~約160%大きい、約75%大きい~約140%大きい、約75%大きい~約120%大きい、約75%大きい~約100%大きい、約75%大きい~約95%大きい、約75%大きい~約90%大きい、約75%大きい~約85%大きい、約75%大きい~約80%大きい、約80%大きい~約10,000%大きい、約80%大きい~約9,000%大きい、約80%大きい~約8,000%大きい、約80%大きい~約7,000%大きい、約80%大きい~約6,000%大きい、約80%大きい~約5,000%大きい、約80%大きい~約4,000%大きい、約80%大きい~約3,000%大きい、約80%大きい~約2,000%大きい、約80%大きい~約1,000%大きい、約80%大きい~約500%大きい、約80%大きい~約480%大きい、約80%大きい~約460%大きい、約80%大きい~約440%大きい、約80%大きい~約420%大きい、約80%大きい~約400%大きい、約80%大きい~約380%大きい、約80%大きい~約360%大きい、約80%大きい~約340%大きい、約80%大きい~約320%大きい、約80%大きい~約300%大きい、約80%大きい~約280%大きい、約80%大きい~約260%大きい、約80%大きい~約240%大きい、約80%大きい~約220%大きい、約80%大きい~約200%大きい、約80%大きい~約180%大きい、約80%大きい~約160%大きい、約80%大きい~約140%大きい、約80%大きい~約120%大きい、約80%大きい~約100%大きい、約80%大きい~約95%大きい、約80%大きい~約90%大きい、約80%大きい~約85%大きい、約85%大きい~約10,000%大きい、約85%大きい~約9,000%大きい、約85%大きい~約8,000%大きい、約85%大きい~約7,000%大きい、約85%大きい~約6,000%大きい、約85%大きい~約5,000%大きい、約85%大きい~約4,000%大きい、約85%大きい~約3,000%大きい、約85%大きい~約2,000%大きい、約85%大きい~約1,000%大きい、約85%大きい~約500%大きい、約85%大きい~約480%大きい、約85%大きい~約460%大きい、約85%大きい~約440%大きい、約85%大きい~約420%大きい、約85%大きい~約400%大きい、約85%大きい~約380%大きい、約85%大きい~約360%大きい、約85%大きい~約340%大きい、約85%大きい~約320%大きい、約85%大きい~約300%大きい、約85%大きい~約280%大きい、約85%大きい~約260%大きい、約85%大きい~約240%大きい、約85%大きい~約220%大きい、約85%大きい~約200%大きい、約85%大きい~約180%大きい、約85%大きい~約160%大きい、約85%大きい~約140%大きい、約85%大きい~約120%大きい、約85%大きい~約100%大きい、約85%大きい~約95%大きい、約85%大きい~約90%大きい、約90%大きい~約10,000%大きい、約90%大きい~約9,000%大きい、約90%大きい~約8,000%大きい、約90%大きい~約7,000%大きい、約90%大きい~約6,000%大きい、約90%大きい~約5,000%大きい、約90%大きい~約4,000%大きい、約90%大きい~約3,000%大きい、約90%大きい~約2,000%大きい、約90%大きい~約1,000%大きい、約90%大きい~約500%大きい、約90%大きい~約480%大きい、約90%大きい~約460%大きい、約90%大きい~約440%大きい、約90%大きい~約420%大きい、約90%大きい~約400%大きい、約90%大きい~約380%大きい、約90%大きい~約360%大きい、約90%大きい~約340%大きい、約90%大きい~約320%大きい、約90%大きい~約300%大きい、約90%大きい~約280%大きい、約90%大きい~約260%大きい、約90%大きい~約240%大きい、約90%大きい~約220%大きい、約90%大きい~約200%大きい、約90%大きい~約180%大きい、約90%大きい~約160%大きい、約90%大きい~約140%大きい、約90%大きい~約120%大きい、約90%大きい~約100%大きい、約90%大きい~約95%大きい、約95%大きい~約10,000%大きい、約95%大きい~約9,000%大きい、約95%大きい~約8,000%大きい、約95%大きい~約7,000%大きい、約95%大きい~約6,000%大きい、約95%大きい~約5,000%大きい、約95%大きい~約4,000%大きい、約95%大きい~約3,000%大きい、約95%大きい~約2,000%大きい、約95%大きい~約1,000%大きい、約95%大きい~約500%大きい、約95%大きい~約480%大きい、約95%大きい~約460%大きい、約95%大きい~約440%大きい、約95%大きい~約420%大きい、約95%大きい~約400%大きい、約95%大きい~約380%大きい、約95%大きい~約360%大きい、約95%大きい~約340%大きい、約95%大きい~約320%大きい、約95%大きい~約300%大きい、約95%大きい~約280%大きい、約95%大きい~約260%大きい、約95%大きい~約240%大きい、約95%大きい~約220%大きい、約95%大きい~約200%大きい、約95%大きい~約180%大きい、約95%大きい~約160%大きい、約95%大きい~約140%大きい、約95%大きい~約120%大きい、約95%大きい~約100%大きい、約100%大きい~約10,000%大きい、約100%大きい~約9,000%大きい、約100%大きい~約8,000%大きい、約100%大きい~約7,000%大きい、約100%大きい~約6,000%大きい、約100%大きい~約5,000%大きい、約100%大きい~約4,000%大きい、約100%大きい~約3,000%大きい、約100%大きい~約2,000%大きい、約100%大きい~約1,000%大きい、約100%大きい~約500%大きい、約100%大きい~約480%大きい、約100%大きい~約460%大きい、約100%大きい~約440%大きい、約100%大きい~約420%大きい、約100%大きい~約400%大きい、約100%大きい~約380%大きい、約100%大きい~約360%大きい、約100%大きい~約340%大きい、約100%大きい~約320%大きい、約100%大きい~約300%大きい、約100%大きい~約280%大きい、約100%大きい~約260%大きい、約100%大きい~約240%大きい、約100%大きい~約220%大きい、約100%大きい~約200%大きい、約100%大きい~約180%大きい、約100%大きい~約160%大きい、約100%大きい~約140%大きい、約100%大きい~約120%大きい、約120%大きい~約10,000%大きい、約120%大きい~約9,000%大きい、約120%大きい~約8,000%大きい、約120%大きい~約7,000%大きい、約120%大きい~約6,000%大きい、約120%大きい~約5,000%大きい、約120%大きい~約4,000%大きい、約120%大きい~約3,000%大きい、約120%大きい~約2,000%大きい、約120%大きい~約1,000%大きい、約120%大きい~約500%大きい、約120%大きい~約480%大きい、約120%大きい~約460%大きい、約120%大きい~約440%大きい、約120%大きい~約420%大きい、約120%大きい~約400%大きい、約120%大きい~約380%大きい、約120%大きい~約360%大きい、約120%大きい~約340%大きい、約120%大きい~約320%大きい、約120%大きい~約300%大きい、約120%大きい~約280%大きい、約120%大きい~約260%大きい、約120%大きい~約240%大きい、約120%大きい~約220%大きい、約120%大きい~約200%大きい、約120%大きい~約180%大きい、約120%大きい~約160%大きい、約120%大きい~約140%大きい、約140%大きい~約10,000%大きい、約140%大きい~約9,000%大きい、約140%大きい~約8,000%大きい、約140%大きい~約7,000%大きい、約140%大きい~約6,000%大きい、約140%大きい~約5,000%大きい、約140%大きい~約4,000%大きい、約140%大きい~約3,000%大きい、約140%大きい~約2,000%大きい、約140%大きい~約1,000%大きい、約140%大きい~約500%大きい、約140%大きい~約480%大きい、約140%大きい~約460%大きい、約140%大きい~約440%大きい、約140%大きい~約420%大きい、約140%大
きい~約400%大きい、約140%大きい~約380%大きい、約140%大きい~約360%大きい、約140%大きい~約340%大きい、約140%大きい~約320%大きい、約140%大きい~約300%大きい、約140%大きい~約280%大きい、約140%大きい~約260%大きい、約140%大きい~約240%大きい、約140%大きい~約220%大きい、約140%大きい~約200%大きい、約140%大きい~約180%大きい、約140%大きい~約160%大きい、約160%大きい~約10,000%大きい、約160%大きい~約9,000%大きい、約160%大きい~約8,000%大きい、約160%大きい~約7,000%大きい、約160%大きい~約6,000%大きい、約160%大きい~約5,000%大きい、約160%大きい~約4,000%大きい、約160%大きい~約3,000%大きい、約160%大きい~約2,000%大きい、約160%大きい~約1,000%大きい、約160%大きい~約500%大きい、約160%大きい~約480%大きい、約160%大きい~約460%大きい、約160%大きい~約440%大きい、約160%大きい~約420%大きい、約160%大きい~約400%大きい、約160%大きい~約380%大きい、約160%大きい~約360%大きい、約160%大きい~約340%大きい、約160%大きい~約320%大きい、約160%大きい~約300%大きい、約160%大きい~約280%大きい、約160%大きい~約260%大きい、約160%大きい~約240%大きい、約160%大きい~約220%大きい、約160%大きい~約200%大きい、約160%大きい~約180%大きい、約180%大きい~約10,000%大きい、約180%大きい~約9,000%大きい、約180%大きい~約8,000%大きい、約180%大きい~約7,000%大きい、約180%大きい~約6,000%大きい、約180%大きい~約5,000%大きい、約180%大きい~約4,000%大きい、約180%大きい~約3,000%大きい、約180%大きい~約2,000%大きい、約180%大きい~約1,000%大きい、約180%大きい~約500%大きい、約180%大きい~約480%大きい、約180%大きい~約460%大きい、約180%大きい~約440%大きい、約180%大きい~約420%大きい、約180%大きい~約400%大きい、約180%大きい~約380%大きい、約180%大きい~約360%大きい、約180%大きい~約340%大きい、約180%大きい~約320%大きい、約180%大きい~約300%大きい、約180%大きい~約280%大きい、約180%大きい~約260%大きい、約180%大きい~約240%大きい、約180%大きい~約220%大きい、約180%大きい~約200%大きい、約200%大きい~約10,000%大きい、約200%大きい~約9,000%大きい、約200%大きい~約8,000%大きい、約200%大きい~約7,000%大きい、約200%大きい~約6,000%大きい、約200%大きい~約5,000%大きい、約200%大きい~約4,000%大きい、約200%大きい~約3,000%大きい、約200%大きい~約2,000%大きい、約200%大きい~約1,000%大きい、約200%大きい~約500%大きい、約200%大きい~約480%大きい、約200%大きい~約460%大きい、約200%大きい~約440%大きい、約200%大きい~約420%大きい、約200%大きい~約400%大きい、約200%大きい~約380%大きい、約200%大きい~約360%大きい、約200%大きい~約340%大きい、約200%大きい~約320%大きい、約200%大きい~約300%大きい、約200%大きい~約280%大きい、約200%大きい~約260%大きい、約200%大きい~約240%大きい、約200%大きい~約220%大きい、約220%大きい~約10,000%大きい、約220%大きい~約9,000%大きい、約220%大きい~約8,000%大きい、約220%大きい~約7,000%大きい、約220%大きい~約6,000%大きい、約220%大きい~約5,000%大きい、約220%大きい~約4,000%大きい、約220%大きい~約3,000%大きい、約220%大きい~約2,000%大きい、約220%大きい~約1,000%大きい、約220%大きい~約500%大きい、約220%大きい~約480%大きい、約220%大きい~約460%大きい、約220%大きい~約440%大きい、約220%大きい~約420%大きい、約220%大きい~約400%大きい、約220%大きい~約380%大きい、約220%大きい~約360%大きい、約220%大きい~約340%大きい、約220%大きい~約320%大きい、約220%大きい~約300%大きい、約220%大きい~約280%大きい、約220%大きい~約260%大きい、約220%大きい~約240%大きい、約240%大きい~約10,000%大きい、約240%大きい~約9,000%大きい、約240%大きい~約8,000%大きい、約240%大きい~約7,000%大きい、約240%大きい~約6,000%大きい、約240%大きい~約5,000%大きい、約240%大きい~約4,000%大きい、約240%大きい~約3,000%大きい、約240%大きい~約2,000%大きい、約240%大きい~約1,000%大きい、約240%大きい~約500%大きい、約240%大きい~約480%大きい、約240%大きい~約460%大きい、約240%大きい~約440%大きい、約240%大きい~約420%大きい、約240%大きい~約400%大きい、約240%大きい~約380%大きい、約240%大きい~約360%大きい、約240%大きい~約340%大きい、約240%大きい~約320%大きい、約240%大きい~約300%大きい、約240%大きい~約280%大きい、約240%大きい~約260%大きい、約260%大きい~約10,000%大きい、約260%大きい~約9,000%大きい、約260%大きい~約8,000%大きい、約260%大きい~約7,000%大きい、約260%大きい~約6,000%大きい、約260%大きい~約5,000%大きい、約260%大きい~約4,000%大きい、約260%大きい~約3,000%大きい、約260%大きい~約2,000%大きい、約260%大きい~約1,000%大きい、約260%大きい~約500%大きい、約260%大きい~約480%大きい、約260%大きい~約460%大きい、約260%大きい~約440%大きい、約260%大きい~約420%大きい、約260%大きい~約400%大きい、約260%大きい~約380%大きい、約260%大きい~約360%大きい、約260%大きい~約340%大きい、約260%大きい~約320%大きい、約260%大きい~約300%大きい、約260%大きい~約280%大きい、約280%大きい~約10,000%大きい、約280%大きい~約9,000%大きい、約280%大きい~約8,000%大きい、約280%大きい~約7,000%大きい、約280%大きい~約6,000%大きい、約280%大きい~約5,000%大きい、約280%大きい~約4,000%大きい、約280%大きい~約3,000%大きい、約280%大きい~約2,000%大きい、約280%大きい~約1,000%大きい、約280%大きい~約500%大きい、約280%大きい~約480%大きい、約280%大きい~約460%大きい、約280%大きい~約440%大きい、約280%大きい~約420%大きい、約280%大きい~約400%大きい、約280%大きい~約380%大きい、約280%大きい~約360%大きい、約280%大きい~約340%大きい、約280%大きい~約320%大きい、約280%大きい~約300%大きい、約300%大きい~約10,000%大きい、約300%大きい~約9,000%大きい、約300%大きい~約8,000%大きい、約300%大きい~約7,000%大きい、約300%大きい~約6,000%大きい、約300%大きい~約5,000%大きい、約300%大きい~約4,000%大きい、約300%大きい~約3,000%大きい、約300%大きい~約2,000%大きい、約300%大きい~約1,000%大きい、約300%大きい~約500%大きい、約300%大きい~約480%大きい、約300%大きい~約460%大きい、約300%大きい~約440%大きい、約300%大きい~約420%大きい、約300%大きい~約400%大きい、約300%大きい~約380%大きい、約300%大きい~約360%大きい、約300%大きい~約340%大きい、約300%大きい~約320%大きい、約320%大きい~約10,000%大きい、約320%大きい~約9,000%大きい、約320%大きい~約8,000%大きい、約320%大きい~約7,000%大きい、約320%大きい~約6,000%大きい、約320%大きい~約5,000%大きい、約320%大きい~約4,000%大きい、約320%大きい~約3,000%大きい、約320%大きい~約2,000%大きい、約320%大きい~約1,000%大きい、約320%大きい~約500%大きい、約320%大きい~約480%大きい、約320%大きい~約460%大きい、約320%大きい~約440%大きい、約320%大きい~約420%大きい、約320%大きい~約400%大きい、約320%大きい~約380%大きい、約320%大きい~約360%大きい、約320%大きい~約340%大きい、約340%大きい~約10,000%大きい、約340%大きい~約9,000%大きい、約340%大きい~約8,000%大きい、約340%大きい~約7,000%大きい、約340%大きい~約6,000%大きい、約340%大きい~約5,000%大きい、約340%大きい~約4,000%大きい、約340%大きい~約3,000%大きい、約340%大きい~約2,000%大きい、約340%大きい~約1,000%大きい、約340%大きい~約500%大きい、約340%大きい~約480%大きい、約340%大きい~約460%大きい、約340%大きい~約440%大きい、約340%大きい~約420%大きい、約340%大きい~約400%大きい、約340%大きい~約380%大きい、約340%大きい~約360%大きい、約360%大きい~約10,000%大きい、約360%大きい~約9,000%大きい、約360%大きい~約8,000%大きい、約360%大きい~約7,000%大きい、約360%大きい~約6,000%大きい、約360%大きい~約5,000%大きい、約360%大きい~約4,000%大きい、約360%大きい~約3,000%大きい、約360%大きい~約2,000%大きい、約360%大きい~約1,000%大きい、約360%大きい~約500%大きい、約360%大きい~約480%大きい、約360%大きい~約460%大きい、約360%大きい~約440%大きい、約360%大きい~約420%大きい、約360%大きい~約400%大きい、約360%大きい~約380%大きい、約380%大きい~約10,000%大きい、約380%大きい~約9,000%大きい、約380%大きい~約8,000%大きい、約380%大きい~約7,000%大きい、約380%大きい~約6,000%大きい、約380%大きい~約5,000%大きい、約380%大きい~約4,000%大きい、約380%大きい~約3,000%大きい、約380%大きい~約2,000%大きい、約380%大きい~約1,000%大きい、約380%大きい~約500%大きい、約380%大きい~約480%大きい、約380%大きい~約460%大きい、約380%大きい~約440%大きい、約380%大きい~約420%大きい、約380%大きい~約400%大
きい、約400%大きい~約10,000%大きい、約400%大きい~約9,000%大きい、約400%大きい~約8,000%大きい、約400%大きい~約7,000%大きい、約400%大きい~約6,000%大きい、約400%大きい~約5,000%大きい、約400%大きい~約4,000%大きい、約400%大きい~約3,000%大きい、約400%大きい~約2,000%大きい、約400%大きい~約1,000%大きい、約400%大きい~約500%大きい、約400%大きい~約480%大きい、約400%大きい~約460%大きい、約400%大きい~約440%大きい、約400%大きい~約420%大きい、約420%大きい~約10,000%大きい、約420%大きい~約9,000%大きい、約420%大きい~約8,000%大きい、約420%大きい~約7,000%大きい、約420%大きい~約6,000%大きい、約420%大きい~約5,000%大きい、約420%大きい~約4,000%大きい、約420%大きい~約3,000%大きい、約420%大きい~約2,000%大きい、約420%大きい~約1,000%大きい、約420%大きい~約500%大きい、約420%大きい~約480%大きい、約420%大きい~約460%大きい、約420%大きい~約440%大きい、約440%大きい~約10,000%大きい、約440%大きい~約9,000%大きい、約440%大きい~約8,000%大きい、約440%大きい~約7,000%大きい、約440%大きい~約6,000%大きい、約440%大きい~約5,000%大きい、約440%大きい~約4,000%大きい、約440%大きい~約3,000%大きい、約440%大きい~約2,000%大きい、約440%大きい~約1,000%大きい、約440%大きい~約500%大きい、約440%大きい~約480%大きい、約440%大きい~約460%大きい、約460%大きい~約10,000%大きい、約460%大きい~約9,000%大きい、約460%大きい~約8,000%大きい、約460%大きい~約7,000%大きい、約460%大きい~約6,000%大きい、約460%大きい~約5,000%大きい、約460%大きい~約4,000%大きい、約460%大きい~約3,000%大きい、約460%大きい~約2,000%大きい、約460%大きい~約1,000%大きい、約460%大きい~約500%大きい、約460%大きい~約480%大きい、約480%大きい~約10,000%大きい、約480%大きい~約9,000%大きい、約480%大きい~約8,000%大きい、約480%大きい~約7,000%大きい、約480%大きい~約6,000%大きい、約480%大きい~約5,000%大きい、約480%大きい~約4,000%大きい、約480%大きい~約3,000%大きい、約480%大きい~約2,000%大きい、約480%大きい~約1,000%大きい、約480%大きい~約500%大きい、約500%大きい~約10,000%大きい、約500%大きい~約9,000%大きい、約500%大きい~約8,000%大きい、約500%大きい~約7,000%大きい、約500%大きい~約6,000%大きい、約500%大きい~約5,000%大きい、約500%大きい~約4,000%大きい、約500%大きい~約3,000%大きい、約500%大きい~約2,000%大きい、約500%大きい~約1,000%大きい、約1,000%大きい~約10,000%大きい、約1,000%大きい~約9,000%大きい、約1,000%大きい~約8,000%大きい、約1,000%大きい~約7,000%大きい、約1,000%大きい~約6,000%大きい、約1,000%大きい~約5,000%大きい、約1,000%大きい~約4,000%大きい、約1,000%大きい~約3,000%大きい、約1,000%大きい~約2,000%大きい、約2,000%大きい~約10,000%大きい、約2,000%大きい~約9,000%大きい、約2,000%大きい~約8,000%大きい、約2,000%大きい~約7,000%大きい、約2,000%大きい~約6,000%大きい、約2,000%大きい~約5,000%大きい、約2,000%大きい~約4,000%大きい、約2,000%大きい~約3,000%大きい、約3,000%大きい~約10,000%大きい、約3,000%大きい~約9,000%大きい、約3,000%大きい~約8,000%大きい、約3,000%大きい~約7,000%大きい、約3,000%大きい~約6,000%大きい、約3,000%大きい~約5,000%大きい、約3,000%大きい~約4,000%大きい、約4,000%大きい~約10,000%大きい、約4,000%大きい~約9,000%大きい、約4,000%大きい~約8,000%大きい、約4,000%大きい~約7,000%大きい、約4,000%大きい~約6,000%大きい、約4,000%大きい~約5,000%大きい、約5,000%大きい~約10,000%大きい、約5,000%大きい~約9,000%大きい、約5,000%大きい~約8,000%大きい、約5,000%大きい~約7,000%大きい、約5,000%大きい~約6,000%大きい、約6,000%大きい~約10,000%大きい、約6,000%大きい~約9,000%大きい、約6,000%大きい~約8,000%大きい、約6,000%大きい~約7,000%大きい、約7,000%大きい~約10,000%大きい、約7,000%大きい~約9,000%大きい、約7,000%大きい~約8,000%大きい、約8,000%大きい~約10,000%大きい、約8,000%大きい~約9,000%大きい、または約9,000%大きい~約10,000%大きい)。
0pM~約200nM、約30pM~約190nM、約30pM~約180nM、約30pM~約170nM、約30pM~約160nM、約30pM~約150nM、約30pM~約140nM、約30pM~約130nM、約30pM~約120nM、約30pM~約110nM、約30pM~約100nM、約30pM~約95nM、約30pM~約90nM、約30pM~約85nM、約30pM~約80nM、約30pM~約75nM、約30pM~約70nM、約30pM~約65nM、約30pM~約60nM、約30pM~約55nM、約30pM~約50nM、約30pM~約45nM、約30pM~約40nM、約30pM~約35nM、約30pM~約30nM、約30pM~約25nM、約30pM~約20nM、約30pM~約15nM、約30pM~約10nM、約30pM~約5nM、約30pM~約2nM、約30pM~約1nM、約30pM~約950pM、約30pM~約900pM、約30pM~約850pM、約30pM~約800pM、約30pM~約750pM、約30pM~約700pM、約30pM~約650pM、約30pM~約600pM、約30pM~約550pM、約30pM~約500pM、約30pM~約450pM、約30pM~約400pM、約30pM~約350pM、約30pM~約300pM、約30pM~約250pM、約30pM~約200pM、約30pM~約150pM、約30pM~約100pM、約30pM~約90pM、約30pM~約80pM、約30pM~約70pM、約30pM~約60pM、約30pM~約50pM、約30pM~約40pM、約40pM~約5μM、約40pM~約2μM、約40pM~約1μM、約40pM~約500nM、約40pM~約250nM、約40pM~約240nM、約40pM~約230nM、約40pM~約220nM、約40pM~約210nM、約40pM~約200nM、約40pM~約190nM、約40pM~約180nM、約40pM~約170nM、約40pM~約160nM、約40pM~約150nM、約40pM~約140nM、約40pM~約130nM、約40pM~約120nM、約40pM~約110nM、約40pM~約100nM、約40pM~約95nM、約40pM~約90nM、約40pM~約85nM、約40pM~約80nM、約40pM~約75nM、約40pM~約70nM、約40pM~約65nM、約40pM~約60nM、約40pM~約55nM、約40pM~約50nM、約40pM~約45nM、約40pM~約40nM、約40pM~約35nM、約40pM~約30nM、約40pM~約25nM、約40pM~約30nM、約40pM~約15nM、約40pM~約10nM、約40pM~約5nM、約40pM~約2nM、約40pM~約1nM、約40pM~約950pM、約40pM~約900pM、約40pM~約850pM、約40pM~約800pM、約40pM~約750pM、約40pM~約700pM、約40pM~約650pM、約40pM~約600pM、約40pM~約550pM、約40pM~約500pM、約40pM~約450pM、約40pM~約400pM、約40pM~約350pM、約40pM~約300pM、約40pM~約250pM、約40pM~約200pM、約40pM~約150pM、約40pM~約100pM、約40pM~約90pM、約40pM~約80pM、約40pM~約70pM、約40pM~約60pM、約40pM~約50pM、約50pM~約5μM、約50pM~約2μM、約50pM~約1μM、約50pM~約500nM、約50pM~約250nM、約50pM~約240nM、約50pM~約230nM、約50pM~約220nM、約50pM~約210nM、約50pM~約200nM、約50pM~約190nM、約50pM~約180nM、約50pM~約170nM、約50pM~約160nM、約50pM~約150nM、約50pM~約140nM、約50pM~約130nM、約50pM~約120nM、約50pM~約110nM、約50pM~約100nM、約50pM~約95nM、約50pM~約90nM、約50pM~約85nM、約50pM~約80nM、約50pM~約75nM、約50pM~約70nM、約50pM~約65nM、約50pM~約60nM、約50pM~約55nM、約50pM~約50nM、約50pM~約45nM、約50pM~約40nM、約50pM~約35nM、約50pM~約30nM、約50pM~約25nM、約50pM~約30nM、約50pM~約15nM、約50pM~約10nM、約50pM~約5nM、約50pM~約2nM、約50pM~約1nM、約50pM~約950pM、約50pM~約900pM、約50pM~約850pM、約50pM~約800pM、約50pM~約750pM、約50pM~約700pM、約50pM~約650pM、約50pM~約600pM、約50pM~約550pM、約50pM~約500pM、約50pM~約450pM、約50pM~約400pM、約50pM~約350pM、約50pM~約300pM、約50pM~約250pM、約50pM~約200pM、約50pM~約150pM、約50pM~約100pM、約50pM~約90pM、約50pM~約80pM、約50pM~約70pM、約50pM~約60pM、約60pM~約5μM、約60pM~約2μM、約60pM~約1μM、約60pM~約500nM、約60pM~約250nM、約60pM~約240nM、約60pM~約230nM、約60pM~約220nM、約60pM~約210nM、約60pM~約200nM、約60pM~約190nM、約60pM~約180nM、約60pM~約170nM、約60pM~約160nM、約60pM~約150nM、約60pM~約140nM、約60pM~約130nM、約60pM~約120nM、約60pM~約110nM、約60pM~約100nM、約60pM~約95nM、約60pM~約90nM、約60pM~約85nM、約60pM~約80nM、約60pM~約75nM、約60pM~約70nM、約60pM~約65nM、約60pM~約60nM、約60pM~約55nM、約60pM~約50nM、約60pM~約45nM、約60pM~約40nM、約60pM~約35nM、約60pM~約30nM、約60pM~約25nM、約60pM~約20nM、約60pM~約15nM、約60pM~約10nM、約60pM~約5nM、約60pM~約2nM、約60pM~約1nM、約60pM~約950pM、約60pM~約900pM、約60pM~約850pM、約60pM~約800pM、約60pM~約750pM、約60pM~約700pM、約60pM~約650pM、約60pM~約600pM、約60pM~約550pM、約60pM~約500pM、約60pM~約450pM、約60pM~約400pM、約60pM~約350pM、約60pM~約300pM、約60pM~約250pM、約60pM~約200pM、約60pM~約150pM、約60pM~約100pM、約60pM~約90pM、約60pM~約80pM、約60pM~約70pM、約70pM~約5μM、約70pM~約2μM、約70pM~約1μM、約70pM~約500nM、約70pM~約250nM、約70pM~約240nM、約70pM~約230nM、約70pM~約220nM、約70pM~約210nM、約70pM~約200nM、約70pM~約190nM、約70pM~約180nM、約70pM~約170nM、約70pM~約160nM、約70pM~約150nM、約70pM~約140nM、約70pM~約130nM、約70pM~約120nM、約70pM~約110nM、約70pM~約100nM、約70pM~約95nM、約70pM~約90nM、約70pM~約85nM、約70pM~約80nM、約70pM~約75nM、約70pM~約70nM、約70pM~約65nM、約70pM~約60nM、約70pM~約55nM、約70pM~約50nM、約70pM~約45nM、約70pM~約40nM、約70pM~約35nM、約70pM~約30nM、約70pM~約25nM、約70pM~約20nM、約70pM~約15nM、約70pM~約10nM、約70pM~約5nM、約70pM~約2nM、約70pM~約1nM、約70pM~約950pM、約70pM~約900pM、約70pM~約850pM、約70pM~約800pM、約70pM~約750pM、約70pM~約700pM、約70pM~約650pM、約70pM~約600pM、約70pM~約550pM、約70pM~約500pM、約70pM~約450pM、約70pM~約400pM、約70pM~約350pM、約70pM~約300pM、約70pM~約250pM、約70pM~約200pM、約70pM~約150pM、約70pM~約100pM、約70pM~約90pM、約70pM~約80pM、約80pM~約5μM、約80pM~約2μM、約80pM~約1μM、約80pM~約500nM、約80pM~約250nM、約80pM~約240nM、約80pM~約230nM、約80pM~約220nM、約80pM~約210nM、約80pM~約200nM、約80pM~約190nM、約80pM~約180nM、約80pM~約170nM、約80pM~約160nM、約80pM~約150nM、約80pM~約140nM、約80pM~約130nM、約80pM~約120nM、約80pM~約110nM、約80pM~約100nM、約80pM~約95nM、約80pM~約90nM、約80pM~約85nM、約80pM~約80nM、約80pM~約75nM、約80pM~約70nM、約80pM~約65nM、約80pM~約60nM、約80pM~約55nM、約80pM~約50nM、約80pM~約45nM、約80pM~約40nM、約80pM~約35nM、約80pM~約30nM、約80pM~約25nM、約80pM~約20nM、約80pM~約15nM、約80pM~約10nM、約80pM~約5nM、約80pM~約2nM、約80pM~約1nM、約80pM~約950pM、約80pM~約900pM、約80pM~約850pM、約80pM~約800pM、約80pM~約750pM、約80pM~約700pM、約80pM~約650pM、約80pM~約600pM、約80pM~約550pM、約80pM~約500pM、約80pM~約450pM、約80pM~約400pM、約80pM~約350pM、約80pM~約300pM、約80pM~約250pM、約80pM~約200pM、約80pM~約150pM、約80pM~約100pM、約80pM~約90pM、約90pM~約5μM、約90pM~約2μM、約90pM~約1μM、約90pM~約500nM、約90pM~約250nM、約90pM~約240nM、約90pM~約230nM、約90pM~約220nM、約90pM~約210nM、約90pM~約200nM、約90pM~約190nM、約90pM~約180nM、約90pM~約170nM、約90pM~約160nM、約90pM~約150nM、約90pM~約140nM、約90pM~約130nM、約90pM~約120nM、約90pM~約110nM、約90pM~約100nM、約90pM~約95nM、約90pM~約90nM、約90pM~約85nM、約90pM~約80nM、約90pM~約75nM、約90pM~約70nM、約90pM~約65nM、約90pM~約60nM、約90pM~約55nM、約90pM~約50nM、約90pM~約45nM、約90pM~約40nM、約90pM~約35nM、約90pM~約30nM、約90pM~約25nM、約90pM~約30nM、約90pM~約15nM、約90pM~約10nM、約90pM~約5nM、約90pM~約2nM、約90pM~約1nM、約90pM~約950pM、約90pM~約900pM、約90pM~約850pM、約90pM~約800pM、約90pM
~約750pM、約90pM~約700pM、約90pM~約650pM、約90pM~約600pM、約90pM~約550pM、約90pM~約500pM、約90pM~約450pM、約90pM~約400pM、約90pM~約350pM、約90pM~約300pM、約90pM~約250pM、約90pM~約200pM、約90pM~約150pM、約90pM~約100pM、約100pM~約30nM、約100pM~約25nM、約100pM~約5μM、約100pM~約2μM、約100pM~約1μM、約100pM~約500nM、約100pM~約250nM、約100pM~約240nM、約100pM~約230nM、約100pM~約220nM、約100pM~約210nM、約100pM~約200nM、約100pM~約190nM、約100pM~約180nM、約100pM~約170nM、約100pM~約160nM、約100pM~約150nM、約100pM~約140nM、約100pM~約130nM、約100pM~約120nM、約100pM~約110nM、約100pM~約100nM、約100pM~約95nM、約100pM~約90nM、約100pM~約85nM、約100pM~約80nM、約100pM~約75nM、約100pM~約70nM、約100pM~約65nM、約100pM~約60nM、約100pM~約55nM、約100pM~約50nM、約100pM~約45nM、約100pM~約40nM、約100pM~約35nM、約100pM~約30nM、約100pM~約15nM、約100pM~約10nM、約100pM~約5nM、約100pM~約2nM、約100pM~約1nM、約100pM~約950pM、約100pM~約900pM、約100pM~約850pM、約100pM~約800pM、約100pM~約750pM、約100pM~約700pM、約100pM~約650pM、約100pM~約600pM、約100pM~約550pM、約100pM~約500pM、約100pM~約450pM、約100pM~約400pM、約100pM~約350pM、約100pM~約300pM、約100pM~約250pM、約100pM~約200pM、約100pM~約150pM、約150pM~約5μM、約150pM~約2μM、約150pM~約1μM、約150pM~約500nM、約150pM~約250nM、約150pM~約240nM、約150pM~約230nM、約150pM~約220nM、約150pM~約210nM、約150pM~約200nM、約150pM~約190nM、約150pM~約180nM、約150pM~約170nM、約150pM~約160nM、約150pM~約150nM、約150pM~約140nM、約150pM~約130nM、約150pM~約120nM、約150pM~約110nM、約150pM~約100nM、約150pM~約95nM、約150pM~約90nM、約150pM~約85nM、約150pM~約80nM、約150pM~約75nM、約150pM~約70nM、約150pM~約65nM、約150pM~約60nM、約150pM~約55nM、約150pM~約50nM、約150pM~約45nM、約150pM~約40nM、約150pM~約35nM、約150pM~約30nM、約150pM~約25nM、約150pM~約30nM、約150pM~約15nM、約150pM~約10nM、約150pM~約5nM、約150pM~約2nM、約150pM~約1nM、約150pM~約950pM、約150pM~約900pM、約150pM~約850pM、約150pM~約800pM、約150pM~約750pM、約150pM~約700pM、約150pM~約650pM、約150pM~約600pM、約150pM~約550pM、約150pM~約500pM、約150pM~約450pM、約150pM~約400pM、約150pM~約350pM、約150pM~約300pM、約150pM~約250pM、約150pM~約200pM、約200pM~約5μM、約200pM~約2μM、約200pM~約1μM、約200pM~約500nM、約200pM~約250nM、約200pM~約240nM、約200pM~約230nM、約200pM~約220nM、約200pM~約210nM、約200pM~約200nM、約200pM~約190nM、約200pM~約180nM、約200pM~約170nM、約200pM~約160nM、約200pM~約150nM、約200pM~約140nM、約200pM~約130nM、約200pM~約120nM、約200pM~約110nM、約200pM~約100nM、約200pM~約95nM、約200pM~約90nM、約200pM~約85nM、約200pM~約80nM、約200pM~約75nM、約200pM~約70nM、約200pM~約65nM、約200pM~約60nM、約200pM~約55nM、約200pM~約50nM、約200pM~約45nM、約200pM~約40nM、約200pM~約35nM、約200pM~約30nM、約200pM~約25nM、約200pM~約30nM、約200pM~約15nM、約200pM~約10nM、約200pM~約5nM、約200pM~約2nM、約200pM~約1nM、約200pM~約950pM、約200pM~約900pM、約200pM~約850pM、約200pM~約800pM、約200pM~約750pM、約200pM~約700pM、約200pM~約650pM、約200pM~約600pM、約200pM~約550pM、約200pM~約500pM、約200pM~約450pM、約200pM~約400pM、約200pM~約350pM、約200pM~約300pM、約200pM~約250pM、約300pM~約30nM、約300pM~約25nM、約300pM~約5μM、約300pM~約2μM、約300pM~約1μM、約300pM~約500nM、約300pM~約250nM、約300pM~約240nM、約300pM~約230nM、約300pM~約220nM、約300pM~約210nM、約300pM~約200nM、約300pM~約190nM、約300pM~約180nM、約300pM~約170nM、約300pM~約160nM、約300pM~約150nM、約300pM~約140nM、約300pM~約130nM、約300pM~約120nM、約300pM~約110nM、約300pM~約100nM、約300pM~約95nM、約300pM~約90nM、約300pM~約85nM、約300pM~約80nM、約300pM~約75nM、約300pM~約70nM、約300pM~約65nM、約300pM~約60nM、約300pM~約55nM、約300pM~約50nM、約300pM~約45nM、約300pM~約40nM、約300pM~約35nM、約300pM~約30nM、約300pM~約15nM、約300pM~約10nM、約300pM~約5nM、約300pM~約2nM、約300pM~約1nM、約300pM~約950pM、約300pM~約900pM、約300pM~約850pM、約300pM~約800pM、約300pM~約750pM、約300pM~約700pM、約300pM~約650pM、約300pM~約600pM、約300pM~約550pM、約300pM~約500pM、約300pM~約450pM、約300pM~約400pM、約300pM~約350pM、約400pM~約5μM、約400pM~約2μM、約400pM~約1μM、約400pM~約500nM、約400pM~約250nM、約400pM~約240nM、約400pM~約230nM、約400pM~約220nM、約400pM~約210nM、約400pM~約200nM、約400pM~約190nM、約400pM~約180nM、約400pM~約170nM、約400pM~約160nM、約400pM~約150nM、約400pM~約140nM、約400pM~約130nM、約400pM~約120nM、約400pM~約110nM、約400pM~約100nM、約400pM~約95nM、約400pM~約90nM、約400pM~約85nM、約400pM~約80nM、約400pM~約75nM、約400pM~約70nM、約400pM~約65nM、約400pM~約60nM、約400pM~約55nM、約400pM~約50nM、約400pM~約45nM、約400pM~約40nM、約400pM~約35nM、約400pM~約30nM、約400pM~約25nM、約400pM~約20nM、約400pM~約15nM、約400pM~約10nM、約400pM~約5nM、約400pM~約2nM、約400pM~約1nM、約400pM~約950pM、約400pM~約900pM、約400pM~約850pM、約400pM~約800pM、約400pM~約750pM、約400pM~約700pM、約400pM~約650pM、約400pM~約600pM、約400pM~約550pM、約400pM~約500pM、約500pM~約5μM、約500pM~約2μM、約500pM~約1μM、約500pM~約500nM、約500pM~約250nM、約500pM~約240nM、約500pM~約230nM、約500pM~約220nM、約500pM~約210nM、約500pM~約200nM、約500pM~約190nM、約500pM~約180nM、約500pM~約170nM、約500pM~約160nM、約500pM~約150nM、約500pM~約140nM、約500pM~約130nM、約500pM~約120nM、約500pM~約110nM、約500pM~約100nM、約500pM~約95nM、約500pM~約90nM、約500pM~約85nM、約500pM~約80nM、約500pM~約75nM、約500pM~約70nM、約500pM~約65nM、約500pM~約60nM、約500pM~約55nM、約500pM~約50nM、約500pM~約45nM、約500pM~約40nM、約500pM~約35nM、約500pM~約30nM、約500pM~約25nM、約500pM~約20nM、約500pM~約15nM、約500pM~約10nM、約500pM~約5nM、約500pM~約2nM、約500pM~約1nM、約500pM~約950pM、約500pM~約900pM、約500pM~約850pM、約500pM~約800pM、約500pM~約750pM、約500pM~約700pM、約500pM~約650pM、約500pM~約600pM、約500pM~約550pM、約600pM~約5μM、約600pM~約2μM、約600pM~約1μM、約600pM~約500nM、約600pM~約250nM、約600pM~約240nM、約600pM~約230nM、約600pM~約220nM、約600pM~約210nM、約600pM~約200nM、約600pM~約190nM、約600pM~約180nM、約600pM~約170nM、約600pM~約160nM、約600pM~約150nM、約600pM~約140nM、約600pM~約130nM、約600pM~約120nM、約600pM~約110nM、約600pM~約100nM、約600pM~約95nM、約600pM~約90nM、約600pM~約85nM、約600pM~約80nM、約600pM~約75nM、約600pM~約70nM、約600pM~約65nM、約600pM~約60nM、約600pM~約55nM、約600pM~約50nM、約600pM~約45nM、約600pM~約40nM、約600pM~約35nM、約600pM~約30nM、約600pM~約25nM、約600pM~約20nM、約600pM~約15nM、約600pM~約10nM、約600pM~約5nM、約600pM~約2nM、約600pM~約1nM、約600pM~約950pM、約6
00pM~約900pM、約600pM~約850pM、約600pM~約800pM、約600pM~約750pM、約600pM~約700pM、約600pM~約650pM、約700pM~約5μM、約700pM~約2μM、約700pM~約1μM、約700pM~約500nM、約700pM~約250nM、約700pM~約240nM、約700pM~約230nM、約700pM~約220nM、約700pM~約210nM、約700pM~約200nM、約700pM~約190nM、約700pM~約180nM、約700pM~約170nM、約700pM~約160nM、約700pM~約150nM、約700pM~約140nM、約700pM~約130nM、約700pM~約120nM、約700pM~約110nM、約700pM~約100nM、約700pM~約95nM、約700pM~約90nM、約700pM~約85nM、約700pM~約80nM、約700pM~約75nM、約700pM~約70nM、約700pM~約65nM、約700pM~約60nM、約700pM~約55nM、約700pM~約50nM、約700pM~約45nM、約700pM~約40nM、約700pM~約35nM、約700pM~約30nM、約700pM~約25nM、約700pM~約20nM、約700pM~約15nM、約700pM~約10nM、約700pM~約5nM、約700pM~約2nM、約700pM~約1nM、約700pM~約950pM、約700pM~約900pM、約700pM~約850pM、約700pM~約800pM、約700pM~約750pM、約800pM~約5μM、約800pM~約2μM、約800pM~約1μM、約800pM~約500nM、約800pM~約250nM、約800pM~約240nM、約800pM~約230nM、約800pM~約220nM、約800pM~約210nM、約800pM~約200nM、約800pM~約190nM、約800pM~約180nM、約800pM~約170nM、約800pM~約160nM、約800pM~約150nM、約800pM~約140nM、約800pM~約130nM、約800pM~約120nM、約800pM~約110nM、約800pM~約100nM、約800pM~約95nM、約800pM~約90nM、約800pM~約85nM、約800pM~約80nM、約800pM~約75nM、約800pM~約70nM、約800pM~約65nM、約800pM~約60nM、約800pM~約55nM、約800pM~約50nM、約800pM~約45nM、約800pM~約40nM、約800pM~約35nM、約800pM~約30nM、約800pM~約25nM、約800pM~約20nM、約800pM~約15nM、約800pM~約10nM、約800pM~約5nM、約800pM~約2nM、約800pM~約1nM、約800pM~約950pM、約800pM~約900pM、約800pM~約850pM、約900pM~約5μM、約900pM~約2μM、約900pM~約1μM、約900pM~約500nM、約900pM~約250nM、約900pM~約240nM、約900pM~約230nM、約900pM~約220nM、約900pM~約210nM、約900pM~約200nM、約900pM~約190nM、約900pM~約180nM、約900pM~約170nM、約900pM~約160nM、約900pM~約150nM、約900pM~約140nM、約900pM~約130nM、約900pM~約120nM、約900pM~約110nM、約900pM~約100nM、約900pM~約95nM、約900pM~約90nM、約900pM~約85nM、約900pM~約80nM、約900pM~約75nM、約900pM~約70nM、約900pM~約65nM、約900pM~約60nM、約900pM~約55nM、約900pM~約50nM、約900pM~約45nM、約900pM~約40nM、約900pM~約35nM、約900pM~約30nM、約900pM~約25nM、約900pM~約20nM、約900pM~約15nM、約900pM~約10nM、約900pM~約5nM、約900pM~約2nM、約900pM~約1nM、約900pM~約950pM、約1nM~約5μM、約1nM~約2μM、約1nM~約1μM、約1nM~約500nM、約1nM~約250nM、約1nM~約240nM、約1nM~約230nM、約1nM~約220nM、約1nM~約210nM、約1nM~約200nM、約1nM~約190nM、約1nM~約180nM、約1nM~約170nM、約1nM~約160nM、約1nM~約150nM、約1nM~約140nM、約1nM~約130nM、約1nM~約120nM、約1nM~約110nM、約1nM~約100nM、約1nM~約95nM、約1nM~約90nM、約1nM~約85nM、約1nM~約80nM、約1nM~約75nM、約1nM~約70nM、約1nM~約65nM、約1nM~約60nM、約1nM~約55nM、約1nM~約50nM、約1nM~約45nM、約1nM~約40nM、約1nM~約35nM、約1nM~約30nM、約1nM~約25nM、約1nM~約20nM、約1nM~約15nM、約1nM~約10nM、約1nM~約5nM、約2nM~約5μM、約2nM~約2μM、約2nM~約1μM、約2nM~約500nM、約2nM~約250nM、約2nM~約240nM、約2nM~約230nM、約2nM~約220nM、約2nM~約210nM、約2nM~約200nM、約2nM~約190nM、約2nM~約180nM、約2nM~約170nM、約2nM~約160nM、約2nM~約150nM、約2nM~約140nM、約2nM~約130nM、約2nM~約120nM、約2nM~約110nM、約2nM~約100nM、約2nM~約95nM、約2nM~約90nM、約2nM~約85nM、約2nM~約80nM、約2nM~約75nM、約2nM~約70nM、約2nM~約65nM、約2nM~約60nM、約2nM~約55nM、約2nM~約50nM、約2nM~約45nM、約2nM~約40nM、約2nM~約35nM、約2nM~約30nM、約2nM~約25nM、約2nM~約20nM、約2nM~約15nM、約2nM~約10nM、約2nM~約5nM、約4nM~約5μM、約4nM~約2μM、約4nM~約1μM、約4nM~約500nM、約4nM~約250nM、約4nM~約240nM、約4nM~約230nM、約4nM~約220nM、約4nM~約210nM、約4nM~約200nM、約4nM~約190nM、約4nM~約180nM、約4nM~約170nM、約4nM~約160nM、約4nM~約150nM、約4nM~約140nM、約4nM~約130nM、約4nM~約120nM、約4nM~約110nM、約4nM~約100nM、約4nM~約95nM、約4nM~約90nM、約4nM~約85nM、約4nM~約80nM、約4nM~約75nM、約4nM~約70nM、約4nM~約65nM、約4nM~約60nM、約4nM~約55nM、約4nM~約50nM、約4nM~約45nM、約4nM~約40nM、約4nM~約35nM、約4nM~約30nM、約4nM~約25nM、約4nM~約20nM、約4nM~約15nM、約4nM~約10nM、約4nM~約5nM、約5nM~約5μM、約5nM~約2μM、約5nM~約1μM、約5nM~約500nM、約5nM~約250nM、約5nM~約240nM、約5nM~約230nM、約5nM~約220nM、約5nM~約210nM、約5nM~約200nM、約5nM~約190nM、約5nM~約180nM、約5nM~約170nM、約5nM~約160nM、約5nM~約150nM、約5nM~約140nM、約5nM~約130nM、約5nM~約120nM、約5nM~約110nM、約5nM~約100nM、約5nM~約95nM、約5nM~約90nM、約5nM~約85nM、約5nM~約80nM、約5nM~約75nM、約5nM~約70nM、約5nM~約65nM、約5nM~約60nM、約5nM~約55nM、約5nM~約50nM、約5nM~約45nM、約5nM~約40nM、約5nM~約35nM、約5nM~約30nM、約5nM~約25nM、約5nM~約20nM、約5nM~約15nM、約5nM~約10nM、約10nM~約5μM、約10nM~約2μM、約10nM~約1μM、約10nM~約500nM、約10nM~約250nM、約10nM~約240nM、約10nM~約230nM、約10nM~約220nM、約10nM~約210nM、約10nM~約200nM、約10nM~約190nM、約10nM~約180nM、約10nM~約170nM、約10nM~約160nM、約10nM~約150nM、約10nM~約140nM、約10nM~約130nM、約10nM~約120nM、約10nM~約110nM、約10nM~約100nM、約10nM~約95nM、約10nM~約90nM、約10nM~約85nM、約10nM~約80nM、約10nM~約75nM、約10nM~約70nM、約10nM~約65nM、約10nM~約60nM、約10nM~約55nM、約10nM~約50nM、約10nM~約45nM、約10nM~約40nM、約10nM~約35nM、約10nM~約30nM、約10nM~約25nM、約10nM~約20nM、約10nM~約15nM、約15nM~約5μM、約15nM~約2μM、約15nM~約1μM、約15nM~約500nM、約15nM~約250nM、約15nM~約240nM、約15nM~約230nM、約15nM~約220nM、約15nM~約210nM、約15nM~約200nM、約15nM~約190nM、約15nM~約180nM、約15nM~約170nM、約15nM~約160nM、約15nM~約150nM、約15nM~約140nM、約15nM~約130nM、約15nM~約120nM、約15nM~約110nM、約15nM~約100nM、約15nM~約95nM、約15nM~約90nM、約15nM~約85nM、約15nM~約80nM、約15nM~約75nM、約15nM~約70nM、約15nM~約65nM、約15nM~約60nM、約15nM~約55nM、約15nM~約50nM、約15nM~約45nM、約15nM~約40nM、約15nM~約35nM、約15nM~約30nM、約15nM~約25nM、約15nM~約20nM、約20nM~約5μM、約20nM~約2μM、約20nM~約1μM、約20nM~約500nM、約20nM~約250nM、約20nM~約240nM、約20nM~約230nM、約20nM~約220nM、約20nM~約210nM、約20nM~約200nM、約20nM~約190nM、約20nM~約180nM、約20nM~約170nM、約20nM~約160nM、約20nM~約150nM、約20nM~約140nM、約20nM~約130nM、約20nM~約120nM、約20nM~約110nM、約20nM~約100nM、約20nM~約95nM、約20nM~約90nM、約20nM~約85nM、約20nM~約80nM、約20nM~約75nM、約20nM~約70nM、約20nM~約65nM、約20nM~約60nM、約20nM~約55nM、約20nM~約50nM、約20nM~約45nM、約20nM~約40nM、約20nM~約35nM、約20nM~約30nM、約20nM~約25nM、約25nM~約5μM、約25nM~約2μM、約25nM~約1μM、約25nM~約500nM、約25nM~約250nM、約25nM~約240nM、約25nM~約230nM、約25nM~約220nM、約25nM~約210nM、約25nM~約200nM、約25nM~約190nM、約25nM~約180nM、約25nM~約170nM、約25nM~約160nM、約25nM~約15
0nM、約25nM~約140nM、約25nM~約130nM、約25nM~約120nM、約25nM~約110nM、約25nM~約100nM、約25nM~約95nM、約25nM~約90nM、約25nM~約85nM、約25nM~約80nM、約25nM~約75nM、約25nM~約70nM、約25nM~約65nM、約25nM~約60nM、約25nM~約55nM、約25nM~約50nM、約25nM~約45nM、約25nM~約40nM、約25nM~約35nM、約25nM~約30nM、約30nM~約5μM、約30nM~約2μM、約30nM~約1μM、約30nM~約500nM、約30nM~約250nM、約30nM~約240nM、約30nM~約230nM、約30nM~約220nM、約30nM~約210nM、約30nM~約200nM、約30nM~約190nM、約30nM~約180nM、約30nM~約170nM、約30nM~約160nM、約30nM~約150nM、約30nM~約140nM、約30nM~約130nM、約30nM~約120nM、約30nM~約110nM、約30nM~約100nM、約30nM~約95nM、約30nM~約90nM、約30nM~約85nM、約30nM~約80nM、約30nM~約75nM、約30nM~約70nM、約30nM~約65nM、約30nM~約60nM、約30nM~約55nM、約30nM~約50nM、約30nM~約45nM、約30nM~約40nM、約30nM~約35nM、約40nM~約5μM、約40nM~約2μM、約40nM~約1μM、約40nM~約500nM、約40nM~約250nM、約40nM~約240nM、約40nM~約230nM、約40nM~約220nM、約40nM~約210nM、約40nM~約200nM、約40nM~約190nM、約40nM~約180nM、約40nM~約170nM、約40nM~約160nM、約40nM~約150nM、約40nM~約140nM、約40nM~約130nM、約40nM~約120nM、約40nM~約110nM、約40nM~約100nM、約40nM~約95nM、約40nM~約90nM、約40nM~約85nM、約40nM~約80nM、約40nM~約75nM、約40nM~約70nM、約40nM~約65nM、約40nM~約60nM、約40nM~約55nM、約40nM~約50nM、約40nM~約45nM、約50nM~約5μM、約50nM~約2μM、約50nM~約1μM、約50nM~約500nM、約50nM~約250nM、約50nM~約240nM、約50nM~約230nM、約50nM~約220nM、約50nM~約210nM、約50nM~約200nM、約50nM~約190nM、約50nM~約180nM、約50nM~約170nM、約50nM~約160nM、約50nM~約150nM、約50nM~約140nM、約50nM~約130nM、約50nM~約120nM、約50nM~約110nM、約50nM~約100nM、約50nM~約95nM、約50nM~約90nM、約50nM~約85nM、約50nM~約80nM、約50nM~約75nM、約50nM~約70nM、約50nM~約65nM、約50nM~約60nM、約50nM~約55nM、約60nM~約5μM、約60nM~約2μM、約60nM~約1μM、約60nM~約500nM、約60nM~約250nM、約60nM~約240nM、約60nM~約230nM、約60nM~約220nM、約60nM~約210nM、約60nM~約200nM、約60nM~約190nM、約60nM~約180nM、約60nM~約170nM、約60nM~約160nM、約60nM~約150nM、約60nM~約140nM、約60nM~約130nM、約60nM~約120nM、約60nM~約110nM、約60nM~約100nM、約60nM~約95nM、約60nM~約90nM、約60nM~約85nM、約60nM~約80nM、約60nM~約75nM、約60nM~約70nM、約60nM~約65nM、約70nM~約5μM、約70nM~約2μM、約70nM~約1μM、約70nM~約500nM、約70nM~約250nM、約70nM~約240nM、約70nM~約230nM、約70nM~約220nM、約70nM~約210nM、約70nM~約200nM、約70nM~約190nM、約70nM~約180nM、約70nM~約170nM、約70nM~約160nM、約70nM~約150nM、約70nM~約140nM、約70nM~約130nM、約70nM~約120nM、約70nM~約110nM、約70nM~約100nM、約70nM~約95nM、約70nM~約90nM、約70nM~約85nM、約70nM~約80nM、約70nM~約75nM、約80nM~約5μM、約80nM~約2μM、約80nM~約1μM、約80nM~約500nM、約80nM~約250nM、約80nM~約240nM、約80nM~約230nM、約80nM~約220nM、約80nM~約210nM、約80nM~約200nM、約80nM~約190nM、約80nM~約180nM、約80nM~約170nM、約80nM~約160nM、約80nM~約150nM、約80nM~約140nM、約80nM~約130nM、約80nM~約120nM、約80nM~約110nM、約80nM~約100nM、約80nM~約95nM、約80nM~約90nM、約80nM~約85nM、約90nM~約5μM、約90nM~約2μM、約90 mM~約1μM、約90nM~約500nM、約90nM~約250nM、約90nM~約240nM、約90nM~約230nM、約90nM~約220nM、約90nM~約210nM、約90nM~約200nM、約90nM~約190nM、約90nM~約180nM、約90nM~約170nM、約90nM~約160nM、約90nM~約150nM、約90nM~約140nM、約90nM~約130nM、約90nM~約120nM、約90nM~約110nM、約90nM~約100nM、約90nM~約95nM、約100nM~約5μM、約100nM~約2μM、約100nM~約1μM、約100nM~約500nM、約100nM~約250nM、約100nM~約240nM、約100nM~約230nM、約100nM~約220nM、約100nM~約210nM、約100nM~約200nM、約100nM~約190nM、約100nM~約180nM、約100nM~約170nM、約100nM~約160nM、約100nM~約150nM、約100nM~約140nM、約100nM~約130nM、約100nM~約120nM、約100nM~約110nM、約110nM~約5μM、約110nM~約2μM、約110nM~約1μM、約110nM~約500nM、約110nM~約250nM、約110nM~約240nM、約110nM~約230nM、約110nM~約220nM、約110nM~約210nM、約110nM~約200nM、約110nM~約190nM、約110nM~約180nM、約110nM~約170nM、約110nM~約160nM、約110nM~約150nM、約110nM~約140nM、約110nM~約130nM、約110nM~約120nM、約120nM~約5μM、約120nM~約2μM、約120nM~約1μM、約120nM~約500nM、約120nM~約250nM、約120nM~約240nM、約120nM~約230nM、約120nM~約220nM、約120nM~約210nM、約120nM~約200nM、約120nM~約190nM、約120nM~約180nM、約120nM~約170nM、約120nM~約160nM、約120nM~約150nM、約120nM~約140nM、約120nM~約130nM、約130nM~約5μM、約130nM~約2μM、約130nM~約1μM、約130nM~約500nM、約130nM~約250nM、約130nM~約240nM、約130nM~約230nM、約130nM~約220nM、約130nM~約210nM、約130nM~約200nM、約130nM~約190nM、約130nM~約180nM、約130nM~約170nM、約130nM~約160nM、約130nM~約150nM、約130nM~約140nM、約140nM~約5μM、約140nM~約2μM、約140nM~約1μM、約140nM~約500nM、約140nM~約250nM、約140nM~約240nM、約140nM~約230nM、約140nM~約220nM、約140nM~約210nM、約140nM~約200nM、約140nM~約190nM、約140nM~約180nM、約140nM~約170nM、約140nM~約160nM、約140nM~約150nM、約150nM~約5μM、約150nM~約2μM、約150nM~約1μM、約150nM~約500nM、約150nM~約250nM、約150nM~約240nM、約150nM~約230nM、約150nM~約220nM、約150nM~約210nM、約150nM~約200nM、約150nM~約190nM、約150nM~約180nM、約150nM~約170nM、約150nM~約160nM、約160nM~約5μM、約160nM~約2μM、約160nM~約1μM、約160nM~約500nM、約160nM~約250nM、約160nM~約240nM、約160nM~約230nM、約160nM~約220nM、約160nM~約210nM、約160nM~約200nM、約160nM~約190nM、約160nM~約180nM、約160nM~約170nM、約170nM~約5μM、約170nM~約2μM、約170nM~約1μM、約170nM~約500nM、約170nM~約250nM、約170nM~約240nM、約170nM~約230nM、約170nM~約220nM、約170nM~約210nM、約170nM~約200nM、約170nM~約190nM、約170nM~約180nM、約180nM~約5μM、約180nM~約2μM、約180nM~約1μM、約180nM~約500nM、約180nM~約250nM、約180nM~約240nM、約180nM~約230nM、約180nM~約220nM、約180nM~約210nM、約180nM~約200nM、約180nM~約190nM、約190nM~約5μM、約190nM~約2μM、約190nM~約1μM、約190nM~約500nM、約190nM~約250nM、約190nM~約240nM、約190nM~約230nM、約190nM~約220nM、約190nM~約210nM、約190nM~約200nM、約200nM~約5μM、約200nM~約2μM、約200nM~約1μM、約200nM~約500nM、約200nM~約250nM、約200nM~約240nM、約200nM~約230nM、約200nM~約220nM、約200nM~約210nM、約210nM~約5μM、約210nM~約2μM、約210nM~約1μM、約210nM~約500nM、約210nM~約250nM、約210nM~約240nM、約210nM~約230nM、約210nM~約220nM、約220nM~約5μM、約220nM~約2μM、約220nM~約1μM、約220nM~約500nM、約220nM~約250nM、約220nM~約240nM、約220nM~約230nM、約230nM~約5μM、約230nM~約2μM、約230nM~約1μM、約230nM~約500nM、約230nM~約250nM、約230nM~約240nM、約240nM~約5μM、約240nM~約2μM、約240nM~約1μM、約240nM~約500nM、約240nM~約250nM、約250nM~約5μM、約250nM~約2μM、約250nM~約1μM、約250nM~約500nM、約500nM~約5μM、約500nM~約2μM、約500nM~約1μM、約
1μM~約5μM、約1μM~約2μM、または約2μM~約5μM)である。
400μM~約600μM、約400μM~約500μM、約500μM~約1mM、約500μM~約900μM、約500μM~約800μM、約500μM~約700μM、約500μM~約600μM、約600μM~約1mM、約600μM~約900μM、約600μM~約800μM、約600μM~約700μM、約700μM~約1mM、約700μM~約900μM、約700μM~約800μM、約800μM~約1mM、約800μM~約900μM、または約900μM~約1mMの間)。
いくつかの実施形態では、本発明で提供するABPCは、薬物(例えば、化学療法薬物、小分子)、毒素、または放射性同位体にコンジュゲートすることができる。薬物、毒素、および放射性同位体(例えば、がんの治療に有用であることが知られている)の非限定的な例は、当該技術分野で既知である。
本明細書ではまた、ABPCを発現する組換え細胞(例えば、本明細書に記載のABPCのうちのいずれか)を生成する方法であって、ABPCをコードする核酸を細胞内に導入して、組換え細胞を産生することと、組換え細胞を、ABPCの発現に十分な条件下で培養することと、を含む方法が提供される。いくつかの実施形態では、導入のステップは、ABPCをコードする核酸を含む発現ベクターを細胞内に導入して組換え細胞を産生することを含む。
本発明では、DLL3またはDLL3のエピトープを表面に提示するがん細胞の集団を有することを特徴とするがんを治療する方法であって、治療有効量の本明細書に記載の医薬組成物または本明細書に記載のABPCのうちのいずれかを、がん細胞の集団を有することを特徴とするがんを有すると特定される対象に投与することを含む方法が提供される。
本明細書ではまた、本明細書に記載のABPCのうちの少なくとも1つを含む組成物(例えば、医薬組成物)も提供される。いくつかの実施形態では、組成物(例えば、医薬組成物)は、滅菌バイアルまたは予め充填された注射器に配置され得る。
本明細書ではまた、本明細書に記載のABPCのうちのいずれか、本明細書に記載の組成物のいずれか、または本明細書に記載の医薬組成物のいずれかを含むキットが提供される。いくつかの実施形態では、キットは、本明細書に記載の方法のうちのいずれかを実施するための説明書を含むことができる。いくつかの実施形態では、キットは、本明細書に記載の組成物(例えば、医薬組成物)のうちのいずれかの少なくとも1つの用量を含むことができる。いくつかの実施形態では、キットは、本明細書に記載の医薬組成物のうちのいずれかを投与するための注射器を提供することができる。
また、標的哺乳動物細胞の表面上に提示されるDLL3またはDLL3のエピトープに特異的に結合できる第1の抗原結合ドメインを含むタンパク質構築物(PC)も提供され、(a)pHが約7.0~約8.0の第1の抗原結合ドメイン(または本明細書に記載のこの範囲のいずれかの部分範囲)の解離速度が、pHが約4.0~約6.5(または本明細書に記載のこの範囲のいずれかの部分範囲)での解離速度よりも速く、かつ/または(b)pHが約7.0~約8.0(またはこの範囲のいずれかの部分範囲)の第1の抗原結合ドメインの解離定数(KD)が、pHが約4.0~約6.5でのKDよりも大きい。
本明細書ではまた、抗原結合タンパク質構築物のpH依存性を改善する方法も提供され、本方法は、抗原結合ドメインを含む出発抗原結合タンパク質構築物を提供することと、出発抗原結合タンパク質構築物における抗原結合ドメインの1つ以上のCDRにヒスチジンによる1つ以上のアミノ酸置換を導入することとを含み、本方法は、(a)出発抗原結合タンパク質構築物と比較した場合の、約4.0~約6.5のpHでの抗原結合ドメインの解離速度と約7.0~約8.0のpHでの解離速度との比率の増加(例えば、少なくとも0.1倍の増加~約100倍の増加、または本明細書に記載のこの範囲のいずれかの部分範囲)、および(b)出発抗原結合タンパク質構築物と比較した場合の、約4.0~約6.5のpHでの抗原結合ドメインの解離定数(KD)と約7.0~約8.0のpHでのKDとの比率の増加(例えば、少なくとも0.1倍の増加~約100倍の増加、または本明細書に記載のこの範囲のいずれかの部分範囲)、の一方または両方を有する抗原結合タンパク質構築物の生成をもたらす。
実施形態1は、標的哺乳動物細胞の表面に提示されるDLL3またはDLL3のエピトープに特異的に結合できる第1の抗原結合ドメインを含む有効量の抗原結合タンパク質構築物(ABPC)を含む医薬組成物であり、(a)約4.0~約6.5のpHでの第1の抗原結合ドメインの解離速度は、約7.0~約8.0のpHでの解離速度よりも速いか、または(b)約4.0~約6.5のpHでの第1の抗原結合ドメインの解離定数(KD)は、約7.0~約8.0のpHでのKDよりも大きい。
DLL3に特異的なpH特性改変されたABPCは、2つの方法を用いて作製される。第1のアプローチでは、DLL3に対する公開されたモノクローナル抗体を、DLL3へのpH依存的結合のエンジニアリングを可能にする追加の変異の導入のための出発テンプレートとして使用し、i)コンジュゲートした毒素のエンドリソソーム蓄積の増強、ならびにii)細胞表面へのDLL3リサイクルの増強を行う。第2のアプローチでは、天然ライブラリまたは規定のCDR組成物を有するライブラリからの抗体ディスプレイ方法を介して、DLL3に特異的なpH特性改変されたABPCの選択のために設計された条件下でのスクリーニングを介して、DLL3に特異的なデノボABPCの探索を行う。いずれの場合も、ヒスチジン残基は、pH依存的結合タンパク質を改変する上で重要な役割を果たす。
本明細書で考察されるように、DLL3に特異的なpH特性改変ABPCは、酸性pHでのDLL3結合の減少(例えば、pH5.0、pH5.5)の望ましい特性を示すが、高いpHでの結合の増強(例えば、pH7.4)は、生理学的条件下でのエンドリソソームにおけるそれらの蓄積を増強する。
DLL3に特異的なpH特性改変ABPCが、中性pHで細胞表面DLL3に結合することを実証するために、細胞表面結合アッセイを行う。DLL3+であるヒト細胞のパネルを組み立てる(例えば、NCI-H82NCI-H660、U-118-MG)。所与の細胞株の遺伝子発現(例えば、DLL3)を同定および定量化する方法は、当該技術分野に既知であり、例えば、Cancer Cell Line Encyclopedia(CCLE;https://portals.broadinstitute.org/ccle)を参照して、腫瘍細胞株における所与の遺伝子の発現レベルおよび/または変異状態を確認すること、rtPCR、マイクロアレイ、またはRNA-Seq分析、または当該技術分野で既知の抗体による細胞染色(例えば、R&D Systems Human DLL3 Antibody(AB4315)またはAbcam Recombinant Anti-DLL3 Antibody、DLL3のカタログ番号AB229902)が挙げられる。細胞を150μLのpH7.4培地中にウェルあたりおよそ5~10,000で播種し、1pM~1μMのいくつかの用量(例えば、2倍希釈系列)で、DLL3に特異的な既知の対照ABPC(例えば、抗体、ロバルピツズマブ、SC16.4、SC16.13、SC16.15、SC16.25、SC16.34、SC16.67)、DLL3に特異的なpH特性改変ABPC、および適切な陰性アイソタイプ対照mAb(例えばBiolegend Purified Human IgG1 Isotype Control Recombinant Antibody,カタログ番号403501)のうちの1つと共に37℃で5分間インキュベートする。実験の開始前に、すべての抗体の結合特性を、当該技術分野に既知の方法を使用して検証する。5分間のインキュベートの後、細胞を4%ホルムアルデヒドで固定し(室温で20分)、適切なフルオロフォア標識二次抗体(例えば、ThermoFisherマウス抗ヒトIgG1 Fc二次抗体、AlexaFluor488、カタログ番号A-10631)と共に60分間インキュベートする。非結合試薬を一連のPBS洗浄で洗浄し、共焦点顕微鏡を用いて細胞パネルをイメージングする。画像を解析すると、DLL3に特異的な既知の対照ABPCならびにDLL3に特異的なpH特性改変されたABPCと結合した細胞の表面上で有意な蛍光が観察され得るが、アイソタイプ陰性対照についてはほとんど表面結合が観察されない。表面結合に対するpHの効果を単離するために、同じ実験を2回繰り返し、一次抗体のインキュベートは、順次、より低いpH(例えば、pH6.5、および5.5、および5.0)で行う。得られた共焦点顕微鏡画像の解析により、アイソタイプ陰性対照を除いて試験したすべてのmAbと結合した細胞の表面上で有意な蛍光が示され、この蛍光は、pHが減少するにつれて、DLL3に特異的なpH特性改変ABPCについて減少することを示す。あるいは、フローサイトメトリーによって、当該技術分野で既知の方法を使用して、平均蛍光強度について細胞を分析する。解析される抗体の中性pHでの細胞上の解離定数KDは、当該技術分野で既知である非線形回帰法(例えば、Scatchardプロット)によって決定される。結果をまとめると、pH特性改変プロセスは、その結合特性においてpHに依存するDLL3に特異的なpH特性改変ABPCの作製をもたらし、それは、より酸性のpHと比較し、中性のpHでより効果的に結合することを示すことができる。DLL3に特異的なpH特性改変ABPCのpH依存性を評価する他の方法が当該技術分野で既知であり、例えば、フローサイトメトリーを使用してABPC表面結合を測定することが挙げられる。
DLL3に特異的なpH特性改変ABPCが、中性pHで結合した後、低pHでDLL3を放出することができることを実証するために、上記の細胞表面結合アッセイの変異体を、当技術分野に既知の方法を使用して(例えば、一般に、Gera N.(2012)PLoS ONE7(11):e48928に記載されているように)実施する。簡潔には、適切なDLL3+細胞株(継代数25未満)を採取し、ウェル当たり50,000個の細胞をU底96ウェルマイクロプレートに播種する。pH7.4での結合および二次染色、pH5.0での結合および二次染色、ならびにpH7.4での結合に続くpH5.0での30分間の放出およびpH7.4での二次染色、の3つの条件を試験する。DLL3に特異的なpH特性改変ABPCおよびDLL3に特異的な対照ABPCの両方を試験する。細胞を、試験する条件に応じて、pH7.4または5.0のいずれかで、200μLのFACS緩衝液(3%のウシ胎児血清を含有する1×PBS)で2回洗浄する。精製したタンパク質サンプルを適切なpHのFACS緩衝液に希釈し、細胞に添加し、氷上で1時間結合させる。一次抗体とのインキュベート後、pH7.4およびpH5.0の条件を以前と同様に2回洗浄し、次いで、1:50で希釈した100μlの二次ラット抗ヒトFc AF488(BioLegend 410706)もしくは他の適切な抗体、または1:50で希釈した抗Myc-TagマウスmAb-AF488(Cell Signaling Technologies 2279S)を、適切なpHのFACS緩衝液中に添加し、氷上で30分間インキュベートする。pH5.0放出条件をFACS緩衝液(pH7.4)で2回洗浄した後、100μlのFACS緩衝液(pH5.0)中で再懸濁し、氷上で30分間インキュベートした後、他の条件について記載したように、FACS緩衝液(pH7.4)中で二次染色した。プレートを上記のように2回洗浄し、適切なFACS緩衝液中の1%パラホルムアルデヒド中に再懸濁して、フローサイトメトリー分析のためにそれらを固定する。すべての条件をフローサイトメトリー(Accuri C6、BD Biosciences)上で読み取る。結合は、(平均蛍光強度としての)FLlシグナルの、二次のみに対するシフトとして観察される。データを分析すると、DLL3に特異的なpH特性改変ABPCおよびDLL3に特異的な対照ABPCがDLL3+細胞の表面に中性pHで効果的に結合するが、DLL3に特異的なpH特性改変ABPCがpH5.0では結合が良好でなく、同様に、DLL3に特異的なpH特性改変ABPCがpH7.4では効果的に結合するがpH5.0ではDLL3を放出/結合解除すること、が判断できる。
DLL3に特異的なABPCが細胞取り込み後にエンドリソソーム局在化を行うことを検証および実証するために、当該技術分野に既知の方法(例えば、Mahmutefendic et al.,Int.J.Biochem.Cell Bio.,2011を参照)を用いて内在化アッセイを行う。簡潔には、上記のように、DLL3を発現するヒト細胞のパネルを、当該技術分野において既知の方法を使用して高度に組み立てる。細胞をプレーティングし、PBSで3回洗浄し、中性pHで培地中で37℃で60分間インキュベートし、DLL3に特異的な既知の対照ABPC(例えば、本明細書に記載のもの)、DLL3に特異的なpH特性改変ABPC、および適切な陰性アイソタイプ対照mAb(例えば、本明細書に記載のもの)を、2μg/mlの濃度で添加する。細胞のサブセットにおいて、抗体内在化およびエンドソーム局在化の検証は、当技術分野に既知の方法を使用して行われ、例えば、細胞を、本明細書に記載のように4%ホルムアルデヒド中に固定し、TWEEN20または当技術分野に既知の他の方法(Jamur MC et al(2010)Permeabilization of cell membranes,Methods Mol Biol.588:63-6)を使用して透過させ、エンドソームマーカー、例えば、蛍光RAB11抗体(RAB11抗体、Alexa Fluor 488,3H18L5,ABfinity(商標)Rabbit Monoclonal)で更に染色し、適切な蛍光標識された抗ヒト二次抗体(例えば、本明細書に記載)で染色し、本明細書に記載の共焦点蛍光顕微鏡法を使用してイメージングする。共焦点画像の分析を使用して、DLL3に特異的なpH特性改変ABPC、およびDLL3に特異的な対照ABPCの両方を内在化させ、エンドリソソーム内に蓄積されることを示すことができる。
DLL3に特異的なpH特性改変ABPCによる細胞の処理が、DLL3に特異的なpH特性改変ABPCに曝露された細胞の表面上のDLL3のレベルの検出可能な低減をもたらさないことを示すために、または、上記処理が、DLL3に特異的なpH特性改変ABPCに曝露された細胞の表面上のDLL3のレベルの低減を、DLL3に特異的な対照ABPCと比較してももたらさないことを示すために、フローサイトメトリーを使用して抗原密度試験を行う。簡潔に述べると、DLL3を発現する4.0×10^5個の細胞を、100μL培地中の96ウェルプレート中でウェルごとに播種する。細胞を、1pM~1μMのi)DLL3に特異的なpH特性改変ABPC、ii)DLL3に特異的な第1の対照ABPC、iii)適切なアイソタイプ対照、およびiv)未処理の対照、の滴定で処理する。細胞を、37℃で2時間インキュベートし、その時点で、すべての細胞を、DLL3に特異的な第1の対照ABPCまたはDLL3に特異的なpH特性改変されたABPCのいずれかとは異なる(例えば、細胞に対する競合的結合試験によって決定される)エピトープを有する、DLL3に特異的な200nMのフルオロフォア標識された第2の対照ABPCと、4℃で30分間インキュベートする。この30分間のインキュベートの後、すべての細胞の平均蛍光強度(MFI)を、例えば、フローサイトメトリーを使用して、当業者に既知の方法を使用して読み出す。並行して、MFIの関数として処理細胞の表面上のDLL3の存在を定量するために使用することができる定量的標準曲線を、市販の定量キット(例えば、BD Biosciences PE フィコエリスリン蛍光定量キット、カタログ番号340495)を使用して作成し、その際、定量的標準曲線は、製造業者の指示に従って作成する。細胞表面上のDLL3の絶対数を決定する他の方法は、当該技術分野において既知であり、例えば、放射性同位体標識試薬の使用が挙げられる。データを分析すると、少なくとも1つの抗体濃度において、DLL3に特異的な対照ABPCで処理された細胞は、その表面上のDLL3のレベルの低減をもたらす一方で、DLL3に特異的なpH特性改変されたABPCで処理された細胞は、アイソタイプおよび未処理の対照の両方と比較した場合の、有意に小さな低減をもたらすか、または全く低減させないことが理解できる。
抗原結合タンパク質構築物コンジュゲート(ADC)は、バリン-シトルリン(vc)リンカー(以下、DLL3-IgG-DC)を介して、モノメチルアウリスタチンE(MMAE)に本明細書に記載のDLL3結合IgG(以下、DLL3-IgG)を結合させることにより作製する。抗原結合タンパク質構築物のvcMMAEとのコンジュゲーションは、DLL3-IgGの部分的な還元、続いてマレイミドカプロイル-Val-Cit-PABC-MMAE(vcMMAE)との反応から始まる。DLL3-IgG(20mg/mL)を、TCEP(TCEP:mAbのモル当量は2:1)の添加、続いて0℃で一晩インキュベートにより部分的に還元させる。次いで、還元反応を20℃に加温する。すべてのチオールをコンジュゲートするために、vcMMAEを、最終的なvcMMAE:低減したCysモル比=1:15となるように添加する。コンジュゲーション反応は、10%v/vのDMSOの存在下で実施し、20℃で60分間行う。
DLL3に特異的なpH特性改変ADC(例えば、pH特性改変DLL3-IgG-DC)およびDLL3に特異的な対照ABPC ADC(例えば、対照ABPC DLL3-IgG-DC)の両方の細胞毒性活性は、本明細書に記載の方法を使用して選抜される様々な抗原密度を発現するDLL3+細胞株(例えば、本明細書に記載のような)およびDLL3-細胞株(例えば、A549)、任意選択により、当該技術分野で既知の方法(例えば、Expi293(商標)Expression System Kit ThermoFisher カタログ番号: A14635)を用いてDLL3をトランスフェクトしたHEK293細胞などの組換えDLL3を発現する細胞のパネルに対して別々に評価する。検証の目的のために、使用前に、すべての細胞株を、当該技術分野に既知の方法、例えば、qPCR、フローサイトメトリー、mRNA RPKM、および当該技術分野に既知の抗DLL3抗体(例えば、本明細書に記載のような)を使用した抗体染色を使用して、DLL3の発現について試験し、続いて、蛍光顕微鏡法、免疫組織化学、フローサイトメトリー、ELISA、または当該技術分野に既知の他の方法を使用して染色による可視化を行う。化合物の細胞毒性を評価するために、150μLの培地にウェルあたり約10~40,000で細胞を播種し、次いで、アッセイの開始時に、4回重複して1pM~1μMの化合物のグレード分類された用量で処理する。細胞毒性アッセイを、試験化合物の添加後96時間実施する。50μLのレザズリン色素を、培養の最後の4~6時間の間に各ウェルに添加し、培養終了時の生存細胞を評価する。色素還元は、それぞれ535nmおよび590nmの励起波長および発光波長を用いた蛍光分光法によって決定する。分析の際に、処理された細胞によるレザズリン還元の程度を、未処理の対照細胞のものと比較し、細胞毒性パーセントを決定する。あるいは、WST-8キットを使用して、製造業者の指示に従って細胞毒性を測定する(例えば、Dojindo Molecular Technologies カタログ番号CCK-8)。半最大殺傷が観察される濃度であるIC50は、当該技術分野で知られる曲線適合方法を使用して計算する。データを分析することで、DLL3に特異的なpH特性改変ABPC ADCおよび対照ABPC ADCは、1つ以上のDLL3+細胞株に対して実質的に細胞毒性であるが、DLL3細胞-に対して毒性が低いことが判定できる。DLL3に特異的なpH特性改変ADCは、DLL3に特異的な対照ABPC ADCよりも1つ以上のDLL3+細胞株に対して細胞毒性が高いと判定することもできる。その理由は、a)1つ以上の濃度での殺傷のより高い度合いを示すか、またはb)それらが低いIC50を示すか、またはc)それらが中性pH(本明細書に記載の)で、細胞上の解離定数KDを同じ細胞上のIC50で割って得た高い比率を示すからである。
1.培地中に約104個の細胞(例えば、本明細書に記載のDLL3+細胞)を含有する100μLの細胞培養物のアリコートを、96ウェルの不透明な壁プレートの各ウェルに堆積させる。
2.培地を含むが細胞を含まない対照ウェルを調製する。
3.DLL3に特異的なADCを1pM~1uMの範囲の濃度で試験ウェルに添加し、1~5日間インキュベートする。あるいは、二次ADCアッセイにおいて、100nMの二次ADC試薬(培地中の最終濃度、Moradec カタログ番号αHFc-NC-MMAF)および1pM~1uM(培地中の最終濃度)からの範囲の濃度のDLL3に特異的なABPCを、37℃で30分間予め混合し、予めインキュベートした後、混合物を培地に添加し、1~5日間インキュベートする。
4.プレートを室温に約30分間平衡化する。
5.各ウェルに存在する細胞培養培地の体積に等しい体積のCellTiter-Glo試薬を添加する。
6.内容物をオービタルシェーカー上で2分間混合して、細胞溶解を誘導する。
7.プレートを室温で10分間インキュベートし、発光シグナルを安定させる。
8.発光を、RLU=相対発光単位、としてグラフに記録および報告する。
DLL3に特異的なpH特性改変ADC(例えば、pH特性改変DLL3-IgG-DC)は、DLL3に特異的な対照ABPC ADC(例えば、対照ABPC DLL3-IgG-DC)と比較した場合の、DLL3+細胞における毒素の遊離の増加を示すこともできる。本明細書に記載のDLL3に特異的なpH特性改変されたおよび対照のABPC ADCでDLL3+細胞を処理した後、LC-MS/MS法を使用して、処理したDLL3+細胞におけるMMAEを定量する(Singh,A.P.and Shah,D.K.Drug Metabolism and Disposition 45.11(2017):1120-1132)。エレクトロスプレーインターフェースおよび三重四重質量分析計を備えたLC-MS/MSシステムを使用する。MMAEの検出の際、XBridge BEHアミドカラム(Waters,Milford,MA)を使用し、その際、移動相Aを水として(5mMのギ酸アンモニウムおよび0.1%のギ酸)、移動相Bを95:5のアセトニトリル/水として(0.1%のギ酸および1mMのギ酸アンモニウム)、40℃で0.25mL/分の流速で勾配を用いる。クロマトグラフィーのランの合計持続時間は12分であり、2つのMRMスキャン(718.5/686.5および718.5/152.1amu)をモニターする。内部標準として、重水素化(d8)MMAE(MCE MedChem Express,Monmouth Junction,NJ)を使用する。まず、生体サンプル中の非コンジュゲート型MMAEを定量するための方程式は、各薬剤標準についてのピーク面積を、内部標準について得られたピーク面積で割ることによって導出される。次に、得られたピーク面積比を標準濃度の関数としてプロットし、データポイントを線形回帰を用いて曲線にフィットさせる。得られた標準曲線の予測能力を評価するために、3つのQCサンプルを、標準曲線の下位範囲、中位範囲、および上位範囲に含める。次に、得られた標準曲線を用いて、生物学的サンプル中の観察されたMMAEの濃度を推定する。MMAE濃度の測定の際、処理した細胞サンプルをペレット化し、新鮮な培地中で25万個の細胞/100μLの最終濃度まで再構成する。サンプルをd8-MMAE(1ng/mL)でスパイクした後、2倍体積の氷冷メタノールを添加し、-20℃で45分間の凍結融解サイクルを行う。最終細胞溶解物は、サンプルを13,000rpmで4℃で15分間遠心分離し、続いて上清を収集することによって得る。標準およびQCサンプルの調製のために、新鮮な細胞懸濁液(25万/100μl)を、既知の濃度のMMAEおよび内部標準(d8-MMAE)でスパイクし、その後上記の細胞溶解と同様の手順を行う。次いで、得られた細胞溶解物を蒸発させ、移動相B中で再構成し、LC-MS/MSに注入する。DLL3に特異的なpH特性改変ADCで処理したDLL3+細胞の溶解物中の非コンジュゲートMMAEの濃度は、DLL3に特異的な対照ABPC ADCで処理したDLL3+細胞中の濃度よりも高いことが観察される。
本発明によって記載されるDLL3に特異的なpH特性改変されたABPCの驚くべき態様の1つは、エンドソームまたはリソソーム内のDLL3からのABPCの解離の増加を促進し、対照であるDLL3に特異的なABPCまたはDLL3に特異的ではないABPCと比較した場合の、血清半減期の低下をもたらす能力であると言える。この血清半減期の低下は、DLL3に結合すると、DLL3に特異的なpH特性改変されたABPCが、その細胞内在化の強化に起因して循環から除去される頻度の増加に起因しており、これは、非結合のDLL3に特異的なpH特性改変されたABPCの血清濃度の低下を通じて経時的に観察できる。これらの特性を実証するために、マウスおよび/またはサルにおける一連の動物試験を、DLL3に特異的なpH特性改変されたABPCおよびDLL3に特異的な対照ABPCを使用して、当技術分野に既知の方法(例えば、Gupta,P.,et al.(2016),mAbs,8:5,991-997)を用いて実施する。簡潔には、マウス試験を行う際、DLL3に特異的なpH特性改変ABPCまたはDLL3に特異的な対照ABPCのいずれかの単回静脈内ボーラス投与(例えば、5mg/kg)を、DLL3+細胞株(例えば、本明細書に記載のように)で異種移植された2群のNOD SCIDマウス(例えば、Jackson Labs NOD.CB17-Prkdcscid/J Stock番号:001303)に尾静脈を介して行う。異種移植されたマウスは、100~500万個のDLL3+細胞をインビトロで増殖させ、マウスの右脇腹内に皮下接種することによって作製する。腫瘍のサイズを300mm3で一致させる。腫瘍の長さ(L)および幅(W)の測定を電子キャリパーを介して行い、体積を以下の式に従って計算する。V=L×W^2/2。血液サンプルは、15m、30m、1h、8h、24h、および3d、7d、10d、14d、17d、21d、および28dの各時点での各群からの後眼窩出血を介して採取する。サンプルを処理して血清を採取し、抗体濃度を、ELISAまたは当該技術分野に既知の他の方法(例えば、抗ヒトFc抗体を利用する、例えば、PACアッセイまたはMACアッセイ、Fischer,S.K.et al.(2012),mAbs,4:5,623-631,Jackson ImmunoResearch Labs,カタログ番号109-006-006)を使用して定量化する。DLL3に特異的なpH特性改変ABPCおよびDLL3に特異的な対照ABPCの抗体濃度を時間の関数としてプロットする。データを分析することにより、DLL3に特異的なpH特性改変ABPCは、DLL3に特異的な対照ABPCと比較して著しく短い血清半減期を有することが観察され、それによって、同じ抗原に結合するが、pH依存性が異なる他の同様の結合剤(例えば、DLL3に特異的な対照ABPC)と比較した場合の、エンドソームまたはリソソーム内の解離の増強を促進するDLL3のpH依存性に特異的なpH特性改変ABPCの能力を実証することができる。DLL3に特異的なpH特性改変および対照ABPCがDLL3のマウスホモログと交差反応性である場合、類似の実験を非異種移植マウスで繰り返すことができる。
DLL3+腫瘍に対するDLL3に特異的なpH特性改変ADCの増強された抗腫瘍活性は、DLL3+細胞の皮下異種移植モデルにおいて実証することができる。実験の際、100~500万個のDLL3+細胞をインビトロで増殖させ、雌の免疫不全(例えば、SCID-ベージュまたはNOD SCID)マウスの右脇腹内に、マウス1匹あたり、皮下に接種する。腫瘍のサイズは100~200mm3で一致させ、腹腔内投与(IP)を行う(合計約2~6回の投与で約4~7日ごとに1回投与)。腫瘍の長さ(L)および幅(W)の測定を電子キャリパーを介して行い、体積を以下の式に従って計算する。V=L×W^2/2。DLL3に特異的なpH特性改変ADCまたはDLL3に特異的な対照ABPC ADCのいずれかのボーラス(例えば、5mg/kg)を、尾静脈を介して投与する。腫瘍増殖阻害(TGI)および腫瘍増殖遅延(TGD)および生存率は、同じレジメンでのDLL3に特異的な対照ABPC ADCの投与と比較し、DLL3に特異的なpH特性改変ADCの投与で有意に改善される。
修飾された毒性および内在化特性を有するDLL3に特異的なpH特性改変ABPCを作製するために、DLL3上の2つの異なるエピトープに結合する二重特異性抗体を構築する。二重パラトピック抗体は、高い抗原依存性内在化を示すことができ、したがって、抗体-薬物コンジュゲートなどの用途に有用であることが当該技術分野で知られている(例えば、Li et al(2016)A Biparatopic HER2-Targeting Antibody-Drug Conjugate Induces Tumor Regression in Primary Models Refractory to or Ineligible for HER2-Targeted Therapy,Cancer Cell 29:117-29を参照されたい)。簡潔には、DLL3に特異的なpH特性改変DLL3×DLL3二重特異性二重パラトピックABPCは、DLL3に特異的な2つの異なるpH特性改変ABPCからの軽鎖/重鎖対を使用し、これらのそれぞれを、他のエピトープと重複しないDLL3上の異なるエピトープに結合して構築する。非重複エピトープに結合するDLL3に特異的なpH特性改変ABPCのセットは、例えば、本明細書に記載の方法、または当業者に既知の他の方法を使用して発見する。簡潔には、2つの結合剤を、例えば、Abdiche YN et al(2009)Exploring blocking assays using Octet,ProteOn,and Biacore biosensors,Anal Biochem 386:172-80のような競争結合アッセイによってDLL3上の実質的に異なるエピトープと結合することに基づいて選択する。あるいは、本明細書に記載のように、DLL3に特異的な第1のABPCでトランスフェクトした細胞の細胞培養上清を50μg/mLの抗体発現レベルに正規化し、抗ヒトFcセンサー(Forte Bio)上で捕捉する。ベースラインは、1×動態緩衝液(Forte Bio)を使用して確立し、センサーを、pH7.4で300秒間、1×PBS中の50nMのDLL3(DLL3トランスフェクション上清に特異的な第2のABPC、またはDLL3トランスフェクション上清に特異的な第1のABPCと、37℃で30分間混合および予備インキュベート、いずれも50ug/mLに正規化)と会合させ、会合曲線を生成する。DLL3に特異的な第2のABPCの存在下での会合速度が、DLL3に特異的な第1のABPCの存在下での会合速度よりも著しく速い場合(装置のソフトウェアによって計算されるか、または経時的な会合レベルの上昇によって観察する)、DLL3に特異的な第2のABPCは、DLL3の非重複エピトープに結合すると見なす。任意選択で、各抗体を、DLL3を発現する細胞上のそのエピトープに結合したときのその内在化特性についてスクリーニングし、良好に内在化する抗体を選抜する。細胞の表面上に存在する分子の内在化速度を決定するためのアッセイは、当該技術分野において既知である。例えば、Wiley et al.(1991)J.Biol.Chem.266:11083-11094; and Sorkin and Duex(2010)Curr.Protoc.Cell Biol.Chapter,Unit-15.14; Vainshtein et al.(2015)Pharm Res.32:286-299を参照されたい。選抜した後、重および軽鎖のペアリングについて改変された変異を有する重および軽鎖構築物(Spiess et al.,“Alternative molecular formats and therapeutic applications of bispecific antibodies,”2015)を両方のアームについて合成する。DLL3に特異的な二重特異性ABPCは、例えば、Expi293細胞内で対応する重鎖および軽鎖プラスミドを共発現させることによって産生させる。細胞培養上清を採取し、プロテインA精製に供する。DLL3に特異的なヘテロ二量体ABPCを、イオン交換クロマトグラフィー、疎水性相互作用クロマトグラフィー、および混合モードクロマトグラフィー等の追加の精製ステップを介して、ホモ二量体種から分離する。DLL3に特異的な精製されたpH特性改変DLL3×DLL3二重特異性二重パラトピックABPCは、質量分析を介して特徴解析し、純度およびホモ二量体種の非存在を確認し、サイズ排除クロマトグラフィーを用いて単量体抗原結合タンパク質構築物種の存在を確認する。生成抗体について、DLL3への結合を、Biacore分析を介して確認する。他の二重特異性抗体産生方法は、当該技術分野に既知であり、また、当業者に明らかであるように、二重特異性抗体、例えば、本明細書に記載のDLL3×DLL3二重特異性、DLL3に特異的な二重パラトピックABPCを作製するために使用することができる(例えば、Labrijn et al(2014)“Controlled Fab-arm exchange for the generation of stable bispecific IgG1”Nature Protocols 9:2450-2463,accessed at http://www.nature.com/nprot/journal/v9/n10/abs/nprot.2014.169.html)。あるいは、DLL3に特異的なDLL3xDLL3 ABPCの代わりに、DLL3に特異的なpH特性改変DLL3×結合剤ABPCを、当業者に明らかな同様の方法を使用して構築することができ、結合剤は、当該技術分野で公開されているか、または本明細書または当該技術分野で知られている方法(例えば、ディスプレイベースまたは免疫ベースの方法)等の方法を使用して見出される任意の抗体である。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。本発明者らは、ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、ロバルピツズマブ(重鎖は配列番号1、軽鎖は配列番号2)を選択した。簡潔には、CDR中の重鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、重鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで系統的に置換した(MYT0639~MYT0679)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。重鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの重鎖配列変異体、およびb)対応する出発ABPC軽鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し、変異体のpH依存性を、Octet RED 384装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、細胞培養上清を、25μg/mLの抗体発現レベルに正規化し、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL)と120秒間会合させ、会合曲線を作成した。解離フェーズにおいて、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xMES(100mM MES緩衝液+150mM NaCl+0.05%Tween20)pH5.0を使用して、別々の条件で繰り返した。pH5.0およびpH7.4での出発ABPC抗体およびそれぞれの対応する抗体変異体について、会合および解離相曲線を解析し、2つの基準:a)出発ABPCと比較した、ヒスチジンまたはアラニン置換による、pH5.5での解離の増強(すなわち、より高いkoff値)、およびb)抗体変異体自体における、および出発ABPCとのpH5.0と比較した、pH7.4での解離の低減(すなわち、より低いkoff値)を通知した。pH5.0での解離強化またはpH7.4での解離低減または両方のいずれかを示す重鎖変異体をさらなる解析のために選抜した(例えば、MYT0643、MYT0645、MYT0647~MYT0648、MYT0650-MYT0652、MYT0655~MYT0657、MYT0660、MYT0669~MYT0670、MYT0673、MYT0675、MYT0677、MYT0678)。また、いくつかのヒスチジンおよびアラニン変異は、DLL3結合を有しなかったが(例えば、MYT0649、MYT0654、MYT0671~MYT0672、MYT0676)、他の変異は、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT0639~MYT0642、MYT0644、MYT0646、MYT0653、MYT0658~MYT0659、MYT0661~MYT0668、MYT0674、MYT0679)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化しない変異体は、広範囲の変異に耐え、異なる配列を有するが類似した結合特性を有する抗体をもたらし得る重鎖内の位置として留意し、自明でないものとして扱う。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、ロバルピツズマブ(重鎖は配列番号1、軽鎖は配列番号2)を選抜した。簡潔には、CDR中の軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、軽鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで体系的に置換した(MYT1532~MYT1558)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。軽鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの軽鎖配列変異体、およびb)対応する出発ABPC重鎖を共に、当該技術分野で既知の方法を使用しExpi293細胞に同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図2)、変異体のpH依存性を、Octet RED 384装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、5μLの細胞培養上清を195μLの1×PBST(pH7.4)に希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図5に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した軽鎖変異体を、さらなる解析のために選抜した(例えば、MYT1533、MYT1534、MYT1537、MYT1540、MYT1541、MYT1542、MYT1544、MYT1547、MYT1550、MYT1551、MYT1554、MYT1555、MYT1556、MYT1557)。また、いくつかのヒスチジンおよびアラニン変異は、DLL3結合を消失させたが(例えば、MYT1552)、他のものは、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT1532、MYT1535、MYT1536、MYT1538、MYT1539、MYT1543、MYT1545、MYT1546、MYT1548、MYT1549、MYT1553、MYT1558)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、ロバルピツズマブ(重鎖は配列番号1、軽鎖は配列番号2)を選抜した。簡潔には、CDR中の重鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成させるために、実施例9においてさらなる解析のために以前に選抜された重鎖CDR内の個々のアミノ酸変異を、2つ以上のアミノ酸変異として一度に系統的に組み合わせた(MYT1182、MYT1183、MYT1185、MYT1186、MYT1187、MYT1188、MYT1189、MYT1190、MYT1192、MYT1193、MYT1194、MYT1195、MYT1196、MYT1198、MYT1199、MYT1200、MYT1201)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。重鎖CDRに2つ以上のヒスチジンまたはアラニン変異を有する抗体変異形を、a)1つの重鎖組み合わせ配列変異体、およびb)対応する出発ABPC軽鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図3および82)、変異体のpH依存性を、Octet RED 384装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、5μLの細胞培養上清を195μLの1×PBST(pH7.4)に希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図6および83に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した重鎖組み合わせ変異体を、さらなる分析のために選抜した(例えば、MYT1182、MYT1183、MYT1185、MYT1186、MYT1187、MYT1188、MYT1189、MYT1190、MYT1192、MYT1193、MYT1194、MYT1195、MYT1196、MYT1198、MYT1199、MYT1200、MYT1201)。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を操作するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、ロバルピツズマブ(重鎖は配列番号1、軽鎖は配列番号2)を選抜した。簡潔には、CDR中の軽鎖は、Kabat et al(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異型を生成させるために、実施例10で以前にさらなる解析のために選抜された軽鎖CDR内の個々のアミノ酸変異を、2つ以上のアミノ酸変異として一度に系統的に組み合わせた(MYT4262~4281)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。軽鎖CDRに2つ以上のヒスチジンまたはアラニン変異を有する抗体変異形を、a)1つの軽鎖組み合わせ配列変異体、およびb)対応する出発ABPC重鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図12)、変異体のpH依存性を、Octet RED 384またはOctet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図13に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した軽鎖組み合わせ変異体を、さらなる分析のために選抜した(MYT4262~4281)。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を操作するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、ロバルピツズマブ(重鎖は配列番号1、軽鎖は配列番号2)を選抜した。簡潔には、CDR中の重鎖および軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、実施例9~12でさらなる解析のために既に選抜された重鎖および軽鎖CDR内の個々のアミノ酸変異を、2つ以上のアミノ酸変異として一度に系統的に組み合わせた(MYT2800~2845)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。2つ以上のヒスチジンまたはアラニン変異を有する抗体変異体を、a)1つの軽鎖配列変異体、およびb)1つの重鎖配列変異体または重鎖配列変異体の組み合わせを用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図14)、変異体のpH依存性を、Octet RED 384またはOctet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合曲線を生成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図15に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCを比較した)を示した対合された重鎖および軽鎖変異体を、さらなる解析のために選抜した(MYT2800~2845)。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、SC16.4(米国特許第9,089,617B2号)(重鎖は配列番号119、軽鎖は配列番号120)を選択した。簡潔には、CDR中の重鎖は、Kabatetal.(Kabatetal.(1992)SequencesofProteinsofImmunologicalInterest,DIANEpublishing)Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、重鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで系統的に置換した(MYT3048~MYT3084)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。重鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの重鎖配列変異体、およびb)対応する出発ABPC軽鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図23)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20、(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図24に示すように、pH5.4での解離の増強またはpH7.4での解離の低減または両方のいずれか(出発ABPCと比較して)を示した重鎖変異体(MYT3054、MYT3057、MYT3058、MYT3060、MYT3061、MYT3065、MYT3066、MYT3067、MYT3068、MYT3070、MYT3072、MYT3073、MYT3075、MYT3076、MYT3077、MYT3078、MYT3080、MYT3082、MYT3083、およびMYT3084)をさらなる解析のために選抜した。また、いくつかのヒスチジンおよびアラニン変異は、DLL3結合を消失させたが(例えば、MYT3055、MYT3079、およびMYT3081)、他のものは、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3048、MYT3049、MYT3050、MYT3051、MYT3052、MYT3053、MYT3056、MYT3059、MYT3062、MYT3063、MYT3064、MYT3069、MYT3071、およびMYT3074)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目されるが、他には明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を操作するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、SC16.4(米国特許第9,089,617B2号)(重鎖は配列番号119、軽鎖は配列番号120)を選択した。簡潔には、CDR中の軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異形を生成するために、軽鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで体系的に置換した(MYT3085~MYT3110およびMYT4200)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。軽鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの軽鎖配列変異体、およびb)対応する出発ABPC重鎖を共に、当該技術分野で既知の方法を使用しExpi293細胞に同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図25)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合曲線を生成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図26に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した軽鎖変異体を、さらなる分析のために選抜した(例えば、MYT3090、MYT3093、MYT3095、MYT3104、MYT3105、MYT3106、MYT3107、およびMYT3109)。また、ヒスチジンまたはアラニン変異はDLL3結合を消失させなかったが、他のものは、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3085、MYT3086、MYT3087、MYT3088、MYT3089、MYT3091、MYT3092、MYT3094、MYT3096、MYT3097、MYT3098、MYT3099、MYT3100、MYT3101、MYT3102、MYT3103、MYT3108、およびMYT3110)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を操作するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、SC16.4(米国特許第9,089,617B2号)(重鎖は配列番号119、軽鎖は配列番号120)を選択した。簡潔には、CDR中の重鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異型を生成させるために、実施例14で以前にさらなる解析のために選抜された軽鎖CDR内の個々のアミノ酸変異を、2つ以上のアミノ酸変異として一度に系統的に組み合わせた(MYT3399~MYT3424およびMYT4175~MYT4189)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。重鎖CDRに2つ以上のヒスチジンまたはアラニン変異を有する抗体変異形を、a)1つの重鎖組み合わせ配列変異体、およびb)対応する出発ABPC軽鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図27)、変異体のpH依存性を、Octet RED 384装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図28に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した重鎖組み合わせ変異体を、さらなる解析のために選抜した(例えば、MYT3399~MYT3424、MYT4175、MYT4176、MYT4177、MYT4178、MYT4180、MYT4181、MYT4182、MYT4184、MYT4185、およびMYT4187)。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を操作するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、SC16.4(米国特許第9,089,617B2号)(重鎖は配列番号119、軽鎖は配列番号120)を選択した。簡潔には、CDR中の軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異型を生成させるために、実施例15で以前にさらなる解析のために選抜された軽鎖CDR内の個々のアミノ酸変異を、2つ以上のアミノ酸変異として一度に系統的に組み合わせた(MYT4190~4199)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。軽鎖CDRに2つ以上のヒスチジンまたはアラニン変異を有する抗体変異形を、a)1つの軽鎖組み合わせ配列変異体、およびb)対応する出発ABPC重鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図29)、変異体のpH依存性を、Octet RED 384またはOctet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合曲線を生成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図30に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した軽鎖組み合わせ変異体を、さらなる分析のために選抜した(MYT4190-4199)。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を操作するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、SC16.4(米国特許第9,089,617B2号)(重鎖は配列番号119、軽鎖は配列番号120)を選択した。簡潔には、CDR中の重鎖および軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、実施例14~17でさらなる解析のために既に選抜された重鎖および軽鎖CDR内の個々のアミノ酸変異を、2つ以上のアミノ酸変異として一度に系統的に組み合わせた(MYT3493~3513)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。2つ以上のヒスチジンまたはアラニン変異を有する抗体変異形は、当該技術分野において既知の方法を使用して、a)1つの軽鎖配列変異形、およびb)1つの重鎖配列変異形を有するExpi293細胞の同時トランスフェクションによって生成した。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図31)、変異体のpH依存性を、Octet RED 384またはOctet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合曲線を生成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図32に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した対合された重鎖および軽鎖変異体を、さらなる解析のために選抜した(MYT3493~MYT3513)。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.13(US9,089,617B2)(重鎖は配列番号236、軽鎖は配列番号237)を選択した。簡潔には、CDR中の重鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、重鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで系統的に置換した(MYT3182~MYT3225)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。重鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの重鎖配列変異体、およびb)対応する出発ABPC軽鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図33)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図34に示すように、pH5.4での解離の増強またはpH7.4での解離の低減、または両方のいずれか(出発ABPCと比較して)を示した重鎖変異体を、さらなる解析のために選抜した(MYT3183、MYT3185、MYT3187、MYT3189~MYT3194、MYT3196、MYT3197、MYT3198、MYT3200、MYT3202、MYT3210、MYT3212、MYT3214、MYT3218、MYT3220、およびMYT3222)。また、ヒスチジンまたはアラニン変異はDLL3結合を消失させなかったが、他のものは、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3182、MYT3184、MYT3186、MYT3188、MYT3195、MYT3199、MYT3201、MYT3203、MYT3204、MYT3205、MYT3206、MYT3207、MYT3208、MYT3209、MYT3211、MYT3213、MYT3215、MYT3216、MYT3217、MYT3219、MYT3221、MYT3223、MYT3224、およびMYT3225)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.13(US9,089,617B2)(重鎖は配列番号236、軽鎖は配列番号237)を選択した。簡潔には、CDR中の軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、軽鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで体系的に置換した(MYT3226~MYT3251)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。軽鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの軽鎖配列変異体、およびb)対応する出発ABPC重鎖を共に、当該技術分野で既知の方法を使用しExpi293細胞に同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図35)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図36に示すように、pH5.4での解離の増強またはpH7.4での解離の低減、または両方(出発ABPCと比較して)のいずれかを示す軽鎖変異体を、さらなる解析のために選抜した(例えば、MYT3227、MYT3231、MYT3234、MYT3235、MYT3236、MYT3237、MYT3245、MYT3246、MYT3248、およびMYT3250)。また、いくつかのヒスチジンおよびアラニン変異は、DLL3結合を消失させたが(例えば、MYT3249)、他のものは、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3226、MYT3228、MYT3229、MYT3230、MYT3232、MYT3233、MYT3238、MYT3239、MYT3240、MYT3241、MYT3242、MYT3243、MYT3244、MYT3247、およびMYT3251)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.13(米国特許第9,089,617B2号)(重鎖は配列番号236、軽鎖は配列番号237)を選択した。簡潔には、CDR中の重鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異型を生成させるために、実施例19で以前にさらなる解析のために選抜された重鎖CDR内の個々のアミノ酸変異を、2つ以上のアミノ酸変異として一度に系統的に組み合わせた(MYT4346~MYT4371)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。重鎖CDRに2つ以上のヒスチジンまたはアラニン変異を有する抗体変異形を、a)1つの重鎖組み合わせ配列変異体、およびb)対応する出発ABPC軽鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図37)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図38に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した重鎖組み合わせ変異体を、さらなる解析のために選抜した(例えば、MYT4346~MYT4366、MYT4368、MYT4369、およびMYT4370)。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.13(米国特許第9,089,617B2号)(重鎖は配列番号236、軽鎖は配列番号237)を選択した。簡潔には、CDR中の軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異型を生成させるために、実施例20で以前にさらなる解析のために選抜された軽鎖CDR内の個々のアミノ酸変異を、2つ以上のアミノ酸変異として一度に系統的に組み合わせた(MYT4372)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。軽鎖CDRに2つ以上のヒスチジンまたはアラニン変異を有する抗体変異形を、a)1つの軽鎖組み合わせ配列変異体、およびb)対応する出発ABPC重鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図39)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図40に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した軽鎖組み合わせ変異体を、さらなる分析のために選抜した(MYT4372)。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.13(米国特許第9,089,617B2号)(重鎖は配列番号236、軽鎖は配列番号237)を選択した。簡潔には、CDR中の重鎖および軽鎖は、 Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、実施例19~22でさらなる解析のために既に選抜された重鎖および軽鎖CDR内の個々のアミノ酸変異を、2つ以上のアミノ酸変異として一度に系統的に組み合わせた(MYT3526~3551)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。2つ以上のヒスチジンまたはアラニン変異を有する抗体変異形は、当該技術分野において既知の方法を使用して、a)1つの軽鎖配列変異形、およびb)1つの重鎖配列変異形を有するExpi293細胞の同時トランスフェクションによって生成した。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図41)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図42に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した対合された重鎖および軽鎖変異体を、さらなる解析のために選択した(MYT3526~MYT3530、MYT3532、MYT3534、MYT3536~MYT3537、MYT3539~MYT3543、MYT3545、MYT3547、およびMYT3549~3551)。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.15(米国特許第9,089,617B2号)(重鎖は配列番号335、軽鎖は配列番号336)を選択した。簡潔には、CDR中の重鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、重鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで系統的に置換した(MYT3893~3932)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。重鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの重鎖配列変異体、およびb)対応する出発ABPC軽鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図43)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20、(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図44に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した重鎖変異体を、さらなる解析のために選抜した(例えば、MYT3897、MYT3902~MYT3906、MYT3924、およびMYT3927~MYT3931)。また、いくつかのヒスチジンまたはアラニン変異はDLL3結合を消失させたが(例えばMYT3909、MYT3923、MYT3925、およびMYT3926)、他のものは、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3893、MYT3894、MYT3895、MYT3896、MYT3898、MYT3899、MYT3900、MYT3901、MYT3907、MYT3908、MYT3910、MYT3911、MYT3912、MYT3913、MYT3914、MYT3915、MYT3916、MYT3917、MYT3918、MYT3919、MYT3920、MYT3921、MYT3922、およびMYT3932)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.15(米国特許第9,089,617B2号)(重鎖は配列番号335、軽鎖は配列番号336)を選択した。簡潔には、CDR中の軽鎖は、(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、軽鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで体系的に置換した(MYT3933~MYT3956)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。軽鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの軽鎖配列変異体、およびb)対応する出発ABPC重鎖を共に、当該技術分野で既知の方法を使用しExpi293細胞に同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図45)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図46に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した軽鎖変異体を、さらなる分析のために選抜した(例えば、MYT3933、MYT3935、MYT3938、MYT3940、MYT3943、MYT3944、MYT3948~MYT3953、およびMYT3955)。また、ヒスチジンまたはアラニン変異は、DLL3結合を消失させなかったが、他のものは、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3934、MYT3936、MYT3937、MYT3939、MYT3941、MYT3942、MYT3945、MYT3946、MYT3947、MYT3954、およびMYT3956)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.25(米国特許第9,089,617B2号)(重鎖は配列番号401、軽鎖は配列番号402)を選択した。簡潔には、CDR中の重鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、重鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで系統的に置換した(MYT3759~3802)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。重鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの重鎖配列変異体、およびb)対応する出発ABPC軽鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図47)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20、(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図48に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した重鎖変異体を、さらなる解析のために選抜した(MYT3760、MYT3790、MYT3792、MYT3793、MYT3797、およびMYT3798)。また、いくつかのヒスチジンおよびアラニン変異は、DLL3結合を消失させたが(例えば、MYT3789、MYT3795、MYT3799、およびMYT3800)、他の変異は、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3759、MYT3761、MYT3762、MYT3763、MYT3764、MYT3765、MYT3766、MYT3767、MYT3772~3788、MYT3791、MYT3794、MYT3801、およびMYT3802)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.25(米国特許第9,089,617B2号)(重鎖は配列番号401、軽鎖は配列番号402)を選択した。簡潔には、CDR中の軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、軽鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで体系的に置換した(MYT3803~MYT3825)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。軽鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの軽鎖配列変異体、およびb)対応する出発ABPC重鎖を共に、当該技術分野で既知の方法を使用しExpi293細胞に同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図49)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図50に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した軽鎖変異体を、さらなる解析のために選抜した(例えば、MYT3806およびMYT3807)。また、いくつかのヒスチジンおよびアラニン変異は、DLL3結合を消失させたが(例えば、MYT3810、MYT3811、およびMYT3817)、他の変異は、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3803、MYT3804、MYT3812、MYT3813、MYT3814、MYT3815、MYT3816、MYT3818、MYT3820、MYT3821、およびMYT3822)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.34(米国特許第9,089,617B2号)(重鎖は配列番号470、軽鎖は配列番号471)を選択した。簡潔には、CDR中の重鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、重鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで系統的に置換した(MYT3827~MYT3867)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。重鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの重鎖配列変異体、およびb)対応する出発ABPC軽鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図51)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20、(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図52に示すように、pH5.4での解離の増強またはpH7.4での解離の低減、または両方のいずれか(出発ABPCと比較して)を示した重鎖変異体を、さらなる解析のために選抜した(MYT3828、MYT3831、MYT3833、MYT3836、MYT3838、MYT3839、MYT3840、MYT3841、MYT3843、MYT3844、MYT3846、MYT3848、MYT3849、MYT3850、MYT3853、MYT3858、MYT3861、MYT3863、MYT3865、MYT3866、およびMYT3867)。また、いくつかのヒスチジンおよびアラニン変異は、DLL3結合を消失させたが(例えば、MYT3837、MYT3842、MYT3857、MYT3859、MYT3860、およびMYT3864)、他の変異は、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3827、MYT3829、MYT3830、MYT3832、MYT3834、MYT3835、MYT3845、MYT3847、MYT3851、MYT3852、MYT3854、MYT3855、MYT3856、MYT3862)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を改変するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、hSC16.34(米国特許第9,089,617B2号)(重鎖は配列番号470、軽鎖は配列番号471)を選択した。簡潔には、CDR中の軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、軽鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで体系的に置換した(MYT3868~MYT3891)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。軽鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの軽鎖配列変異体、およびb)対応する出発ABPC重鎖を共に、当該技術分野で既知の方法を使用しExpi293細胞に同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図53)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図54に示すように、pH5.4での解離の増強、またはpH7.4での解離の低減、または両方(出発ABPCと比較して)のいずれかを示した軽鎖変異体を、さらなる解析のために選抜した(例えば、MYT3870、MYT3873~MYT3877、MYT3879、MYT3881、MYT3883、MYT3886、MYT3888、MYT3890、およびMYT3891)。また、いくつかのヒスチジンおよびアラニン変異は、DLL3結合を消失させたが(例えば、MYT3885)、他のものは、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3868、MYT3869、MYT3871、MYT3872、MYT3878、MYT3880、MYT3882、MYT3884、
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を操作するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、SC16.67(米国特許第9,089,617B2号)(重鎖は配列番号537、軽鎖は配列番号538)を選択した。簡潔には、CDR中の重鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、重鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで系統的に置換した(MYT3112~MYT3148)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。重鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの重鎖配列変異体、およびb)対応する出発ABPC軽鎖を用いて、当該技術分野で既知の方法を使用してExpi293細胞を同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図55)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20、(pH7.4)を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図56に示すように、pH5.4での解離の増強またはpH7.4での解離の低減または両方のいずれか(出発ABPCと比較して)を示した重鎖変異体を、さらなる解析のために選抜した(MYT3112、MYT3115、MYT3117、MYT3118、MYT3122、MYT3124、MYT3125、MYT3126、MYT3129、MYT3130、MYT3131、MYT3134、MYT3137、MYT3139、MYT3140、MYT3143、MYT3145、MYT3146、およびMYT3148)。また、いくつかのヒスチジンおよびアラニン変異は、DLL3結合を消失させたが(例えば、MYT3119、およびMYT3144)、他のものは、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3113、MYT3114、MYT3116、MYT3127、MYT3128、MYT3133、MYT3135、およびMYT3136)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を操作するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、SC16.67(米国特許第9,089,617B2号)(重鎖は配列番号537、軽鎖は配列番号538)を選択した。簡潔には、CDR中の軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、軽鎖CDR内の個々のアミノ酸残基を、一度に1つのヒスチジンで体系的に置換した(MYT3149~MYT3178)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。軽鎖CDRに1つのヒスチジンまたはアラニン変異のみを有する抗体変異体を、a)1つの軽鎖配列変異体、およびb)対応する出発ABPC重鎖を共に、当該技術分野で既知の方法を使用しExpi293細胞に同時トランスフェクションすることによって生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図57)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図58に示されるように、pH5.4での解離の増強またはpH7.4での解離の低減、または両方(出発ABPCと比較して)のいずれかを示した軽鎖変異体を、さらなる解析のために選抜した(例えば、MYT3150、MYT3151、MYT3153、MYT3154、MYT3160、MYT3161、MYT3163、MYT3164、MYT3167、MYT3172、MYT3173、およびMYT3177)。いくつかのヒスチジンおよびアラニン変異は、DLL3結合動態の変化がほとんど(例えば、解離定数KDまたは解離速度の1倍未満の変化)または全くなかった(例えば、MYT3149、MYT3152、MYT3156、MYT3157、MYT3158、MYT3159、MYT3162、MYT3165、MYT3166、MYT3168、MYT3169、MYT3172、MYT3173、MYT3174、MYT3175、MYT3176、およびMYT3178)。特に、ヒスチジンは大きく、正に荷電したアミノ酸であるため、これらの変化のない変異体は、幅広い変異に耐え、異なる配列を有するが、類似した結合特性を有する抗体をもたらし得る軽鎖内の位置として注目され、そうでなければ明らかではない。
複数のDLL3結合モノクローナル抗体が文献に記載されており、pH依存性結合を操作するための鋳型として使用することができる[Saunders LR(2016)“A DLL3-targeted antibody-drug conjugate eradicates high-grade pulmonary neuroendocrine tumor-initiating cells in vivo”Science Translational Medicine 7(302):302ra136]。ヒスチジンスキャニングを介するpH特性改変のためのDLL3結合モノクローナル抗体として、SC16.67(米国特許第9,089,617B2号)(重鎖は配列番号537、軽鎖は配列番号538)を選択した。簡潔には、CDR中の重鎖および軽鎖は、Kabatら(Kabat et al.(1992)Sequences of Proteins of Immunological Interest,DIANE publishing)およびIMGT(Lefranc MP(1999)“The IMGT unique numbering for Immunoglobulins,T cell receptors and Ig-like domains”The Immunologist 7,132-136)に記載の方法を使用して同定し、各CDRについて、KabatおよびIMGT CDR定義のいずれかまたは両方に該当する残基をCDR残基と称した。pH依存性配列変異体を生成するために、実施例30および31においてさらなる解析のために以前に選択されていた重鎖および軽鎖CDR内の個々のアミノ酸変異を、一度に2つ以上体系的に組み合わせた(MYT3514~3525)。出発CDR残基がヒスチジンであった場合は、アラニンに変異させた。2つ以上のヒスチジンまたはアラニン変異を有する抗体変異形は、当該技術分野において既知の方法を使用して、a)1つの軽鎖配列変異形、およびb)1つの重鎖配列変異形を有するExpi293細胞の同時トランスフェクションによって生成した。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図59)、変異体のpH依存性を、Octet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、SDS-PAGEゲルの視覚的試験により決定した変異体の定性的な発現レベルに基づいて細胞培養上清を希釈し、高発現体については、5μLの細胞培養上清を1×PBST(pH7.4)195μLに、中発現体については25μLの細胞培養上清を1×PBST(pH7.4)175μLに、および低発現体については100μLの細胞培養上清を1×PBST(pH7.4)100μLに、希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の50nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4における出発ABPC抗体(置換なし)およびそれぞれの対応する抗体変異体について会合および解離相曲線を調べて、2つの基準:a)出発ABPC(置換なし)と比較した場合の、ヒスチジンまたはアラニン置換による、pH5.4における解離の増強(例えば、より高いkoff値)、およびb)pH5.4におけるその抗体変異体自体と比較した場合の、および出発ABPC(置換なし)と比較した場合の、pH7.4における解離の低減(例えば、より低いkoff値)を通知させた。図60に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方(出発ABPCと比較して)を示した対合された重鎖および軽鎖変異体を、さらなる分析のために選抜した(MYT3514-3525)。
実施例9~32からの選択された抗DLL3pH特性改変抗体変異体を、NCI-H82(DLL3+)細胞における内在化およびエンドリソソーム送達について解析した。NCI-H82細胞(ATCC;HTB-175)を回収し、RPMI-1640培地(ATCC;30-2001)+10%GenClone熱不活性化ウシ胎仔血清(HI FBS)(Genesee Scientific;25-514H)中に再懸濁した。細胞数は、トリパンブルー染色およびCountess II FL自動細胞計数器(Thermofisher; AMQAF1000)を使用して測定した。次いで、細胞を2,000,000細胞/mLに希釈し、50μl/ウェルで96ウェル平底細胞培養プレート(Genesee Scientific;25-109)に播種した。抗DLL3pH特性改変抗体変異体、出発ABPC抗体、対照IgG1アイソタイプ対照(BP0297、Bioxcell)、およびビヒクル対照を、通常の培養培地中で100nMに希釈した後、300nMのZenon pHrodo iFL ヒトIgG標識試薬(ThermoFisher;Z25611)と1:1で混合した。混合物を室温で20分間インキュベートし、続いて50μLを細胞に添加した。細胞、抗DLL3抗体変異体、およびZenon pHrodo iFL ヒトIgG標識試薬の混合物を、37℃、5%CO2で1~24時間インキュベートした。インキュベート後、100μLの氷冷フローサイトメトリー(FC)緩衝液(リン酸緩衝食塩水(PBS)、pH7.4+2mMのエチレンジアミン四酢酸(EDTA)+2%(v/v)のHI FBSを各ウェルに添加する。次いで、細胞を4℃で2000rpmで2分間スピンダウンし、200μLの氷冷FC緩衝液で洗浄し、100μLの氷冷FC緩衝液中に再懸濁した。平均緑色蛍光強度は、BD Accuri C6フローサイトメトリーを使用して検出した。データを、Flowjo解析ソフトウェアを使用して解析した。pHrodo greenは、エンドソームおよびリソソームの低pH環境で蛍光するpH感受性色素であり、したがって、抗体内在化およびエンドリソソーム送達を定量化するために使用することができる。NCI-H82(DLL3+)細胞における、抗DLL3出発ABPC抗体ロバルピツズマブ、SC16.4、hSC16.13、hSC16.15、hSC16.25、hSC16.34、SC16.67およびそれらの変異体の内在化およびエンドリソソソーム送達を、pHrodo緑色平均蛍光強度によって測定した結果を図16に示す。いくつかのpH特性改変抗DLL3抗体変異体は、それらの対応する出発ABPC抗体と比較して平均蛍光強度の増加を示し、IgG1アイソタイプ対照と比較して増加した蛍光または増加した蛍光によって示されるように、低いpHでの解離の増加が細胞内での内在化およびエンドリソソソーム送達の増加をもたらすことを実証した。増加したエンドリソソーム送達は、各棒グラフの上部に示すように、各pH特性改変された抗DLL3抗体変異体について、変異体の平均蛍光強度からIgG対照の平均蛍光強度を減算し、次いですべて、変異体の対応する出発ABPCの平均蛍光強度からIgG対照の平均蛍光強度を引いた数で除算した比率として定量化する。例えば、ロバルピツズマブの抗体変異体であるMYT1182、MYT1183、MYT1193、MYT2808、MYT2829等は、ロバルピツズマブ(MYT0638)と比較した場合の、内在化およびエンドリソソーム送達の増加を示し、同様に、例えば、MYT3078、MYT3410、MYT3413、MYT3419、MYT4176、MYT4184等は、SC16.4の抗体変異体であり、SC16.4(MYT3047)等と比較した場合の、内在化およびエンドリソソーム送達の増加を示す。かかるpH特性改変抗DLL3抗体変異体であって、それらの出発ABPC抗体と比較して平均蛍光強度が増加したものを、さらなる解析のために選抜した(MYT1182、MYT1183、MYT1185、MYT1193、MYT1194、MYT1195、MYT1196、MYT2808、MYT2815、MYT2819、MYT2820、MYT2828、MYT2829、MYT2830、MYT2834,MYT2835、MYT4264、MYT4267、MYT4268、MYT4278、MYT4279、MYT3078、MYT3406、MYT3410、MYT3412、MYT3413、MYT3415、MYT3416、MYT3419、MYT3420、MYT3493、MYT3498、MYT3499、MYT3500、MYT3501、MYT3505、MYT3512、MYT4176、MYT4177、MYT4180、MYT4181、MYT4184)。
ファージディスプレイシステムおよびVHドメインに基づくABPCを有するものを含む複数のABPCディスプレイシステムは、文献に記載されており、パニングを使用してpH特性改変ABPCを選択するためのテンプレートとして使用することができる(Scroter C (2015)“A generic approach to engineer antibody pH switches using combinatorial histidine scanning libraries and yeast display”mAbs,7:1,138-151、Bonvin P (2015)“De novo isolation of antibodies with pH-dependent binding properties”mAbs,7:2,294-302、Traxlmayr P (2014)“Construction of pH-sensitive Her2-binding IgG1-Fc by directed evolution”Biotechnology Journal 9(8):1013-1022、Gera N (2012)“Design of pH sensitive binding proteins from the hyperthermophilic Sso7d scaffold”PLOS ONE 7 (11)e48928)。pH特性改変抗DLL3変異体は、独自のヒト化VHファージディスプレイライブラリをスクリーニングすることによって選抜した。ヒト化VHライブラリを、pH依存性抗DLL3 VHドメインを単離するために、連続して低濃度で3ラウンドの選択において、可溶性組換えヒトDLL3細胞外ドメイン(R&D Systems、カタログ番号9749-DL)に対してスクリーニングした。簡潔には、Dynal M-280ストレプトアビジンビーズとインキュベートすることによって、非特異的結合剤についてライブラリを枯渇させ、結合した抗体を磁石を介して分離し、ヒトDLL3との陽性選抜のために上清を回収した。枯渇したライブラリを、pH7.4でビオチン化組換えヒトDLL3と共に、室温で1~3時間さらにインキュベートした。Dynalストレプトアビジンビーズを混合物に添加して、ヒトDLL3結合抗体を捕捉し、pH7.4の緩衝液で3回洗浄した。結合した抗体を、0.1Mグリシン(pH2.7)を使用してビーズから溶出し、次いで、1M Tris(pH7.4)で中和した。この手順を、低濃度のビオチン化ヒトDLL3、繰り返しの洗浄、およびpH5.0での酢酸ナトリウム緩衝液による溶出を連続して行う操作をラウンド2および3おいて繰り返した。ラウンド3の終わりに濃縮されたpH依存性抗体をファージELISAによって解析し、配列決定し、独自のCDR3アミノ酸配列を有する陽性ヒットをさらなる解析のために選抜した(配列番号606~620)。
pH特性改変された抗DLL3変異体は、Expi293細胞を、ヒトIgG1 Fcに遺伝的に融合された可変重鎖をコードするプラスミドでトランスフェクションすることによって、VH-Fc融合体として、およびExpi293細胞を、a)上の実施例34で選択された可変重鎖領域、およびヒトIgG1アイソタイプに対応する定常領域からなる重鎖、およびb)当該技術分野で既知の方法を使用して、選択されたVHドメインに最も近い配列の重鎖と対合することが以前に知られている軽鎖配列と共トランスフェクションすることによって、IgG変異体として生成させた。4日間タンパク質を発現させた後、細胞培養上清を収集し、SDS-PAGE分析によって定量化し(図17)、変異体のpH依存性を、Octet RED 384またはOctet RED 96e装置において、バイオレイヤー干渉法(BLI)を使用して評価した。簡潔には、5μLの細胞培養上清を195μLの1×PBST(pH7.4)に希釈してセンサーチップに充填した。次いで、希釈した上清を、抗ヒトFcセンサー(Forte Bio)上で捕捉した。ベースラインを、1×PBST(50mMリン酸カリウム緩衝液+150mM NaCl+0.05%Tween20)pH7.4を使用して確立し、センサーを、1×PBST(pH7.4)中の100nMのDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)と120秒間会合させ、会合曲線を作成した。解離フェーズでは、センサー上の抗体-抗原複合体を、1×PBST(pH7.4)に300~600秒間曝露した。ベースライン、会合、および解離を、1xPBST(pH5.4)を使用して、別々の条件で全体を通して繰り返した。pH5.4およびpH7.4で、対応する各抗体変異体について会合および解離相曲線を調べ、2つの基準:a)実施例9~32の他の出発ABPCと比較した場合の、pH5.4での解離の増強(例えば、より高いkoff値)、およびb)抗体変異体自体でのpH5.4と比較した場合の、pH7.4での解離の低減(例えば、より低いkoff値)を通知させた。図18に示すように、pH5.4での解離の増強またはpH7.4での解離の低減のいずれかまたは両方を示したVH-Fcおよび再フォーマットIgG抗体を、さらなる解析のために選抜した(例えば、MYT1047、MYT1048、MYT1050、MYT1053、MYT1054、MYT1055、MYT1056、MYT1057、MYT1060、MYT1061、MYT1062、MYT1063、MYT4373、MYT4374、およびMYT4377)。
DLL3の異なるエピトープに結合するVH-Fc分子を同定するために、Octetを介してサンドイッチ形式の競合結合アッセイを行った。抗ヒト捕捉(AHC)センサーチップを、既知のエピトープ(ロバルピツズマブ、SC16.4またはhSC16.13)を有する抗体の溶液に浸漬し、飽和するまで結合させた。センサーを1×PBST(pH7.4)の緩衝液に戻し、250nMの組換えヒトDLL3(R&D Systems、カタログ番号9749-DL、ロット番号DFSG0719011)をセンサー表面に結合させる前に、安定したベースラインの状態にした。1×PBST(pH7.4)の第2のベースラインステップに続いて、センサーをVH-Fc細胞培養上清に浸漬した。さらなる結合は、別個のエピトープへの結合すると解釈し、一方、結合の欠如は、2つの分子が結合するエピトープについてある程度の重複を有すると解釈した。所与のVH-Fc分子について、最も高い観察シグナルからの50%以上のシグナルの低減を競合として分類した。図19に示すように、試験した14個の変異体のうち8個(MYT1047、MYT1050、MYT1053、MYT1055、MYT1056、MYT1061、MYT1062、およびMYT1063)は、hSC16.13との競合を示し、3個の変異体(MYT1054、MYT1056、およびMYT1060)は、SC16.4との競合を示し、2個の変異体(MYT1048およびMYT1058)は、ロバルピツズマブとの競合を示す。加えて、他の2つの変異体(MYT1052およびMYT1057)は、既知の3つの試験抗体との競合を示さず、それらが異なるエピトープに結合することが確認された。
実施例9~13からの選択された抗DLL3pH特性改変抗体変異体の結合親和性を、NCI-H82細胞上で測定した。ウェル当たり100,000個の細胞を、96ウェルのディープウェルプレート中の900μLのFC緩衝液中に再懸濁した。ロバルピツズマブおよびpH特性改変抗体変異体を、1:3希釈で連続希釈した。100μLの希釈抗体を、最終濃度が約100nM~0.024pMの範囲で各ウェルに添加し、4℃で2時間インキュベートした。インキュベート後、細胞を2000rpmで2分間回転させ、上清を廃棄した。細胞を500μLの氷冷FC緩衝液で2回洗浄し、100μLのFC緩衝液で再懸濁した。次いで、細胞をディープウェルプレートから96ウェルの丸底プレートに移し、2000rpmで2分間回転させ、100μLの10μg/mLのAlexa Fluor 488コンジュゲートヤギ抗ヒトIgG二次抗体(ThermoFisher Scientific、A11013)と30分間インキュベートした。インキュベート後、細胞をFC緩衝液で洗浄し、100μLのFC緩衝液中に再懸濁して、BD Accuri C6フローサイトメトリーで読み取った。図20に示すように、サンプル当たりの各濃度における平均蛍光強度からバックグラウンドを減算してプロットした。結合親和性を、Michaelis-Menten結合動態として仮定して、GraphPad Prismによって解離定数KDとして測定した。MYT1193およびMYT2829は、pM~nM範囲のNCI-H82細胞上の細胞表面DLL3への高親和性結合を示し、pH特性改変によって作製された変異体が、それらの対応する出発ABPC(例えば、ロバルピツズマブ)と比較した場合の、機能的に適切な親和性を保持できることが確認された。解離定数KDが100nM未満の変異体を、さらなる解析のために選抜した。
タンパク質融解温度(Tm)を、ディファレンシャルスキャニング蛍光測定(DSF)を使用して測定した。DSFは、加熱によりタンパク質がアンフォールドするときの、分子Sypro Orange(Thermo Scientific、カタログ番号S6650)からの蛍光シグナルを測定することによって、タンパク質のアンフォールドを可視化する。タンパク質がアンフォールドすると、多くの親水性領域がSypro Orange色素に曝露し、次いでこれらの親水性領域に結合し、シグナルの増加をもたらす。タンパク質のTmは、アンフォールド遷移の最大値の半数値として計算され、Sypro Orangeシグナルの第1の誘導をプロットし、この誘導プロットの局所最大値を見つけることによって可視化することができる。1×PBS(pH7.4)中の20μLのタンパク質サンプルを、5μLの25×Sypro Orangeマスターミックスと混合し、5×Sypro Orangeの最終濃度を得た。サンプルを96ウェルPCRプレート(Thermo Scientific、カタログ番号AB-2400/W)を使用し、光学的カバー(Thermo Scientific、カタログ番号4360954)でシールする。PCRプレートをリアルタイムPCR装置(Thermo Scientific Quant Studio 3)に挿入し、プレート温度を25℃で3分間安定させた後、95℃まで0.2℃刻みでランプし、1秒間安定させた後、Sypro Orangeシグナルを測定した。抗DLL3変異体の融解温度(Tm)値を図21に示す。いくつかの変異型(MYT1185、MYT1193およびMYT2829)は、ロバルピツズマブと同様の融解温度値を示し、すなわち、pH特性改変によって作製された変異体が、それらの対応する出発ABPC(例えば、ロバルピツズマブ)と比較して機能的に適切な熱安定性を保持できることが確認された。対応する出発ABPC(例えば、ロバルピツズマブ)の融解温度から10℃を超える融解温度を有する変異体(MYT1185、MYT1193、およびMYT2829)を、さらなる解析のために選抜した。
細胞内へのDLL3媒介性内在化およびエンドリソソーム送達についての抗DLL3 mAbの特異性を、Raji細胞(DLL3-)内での内在化およびエンドリソソーム送達を測定することにより評価した。簡潔には、細胞を2,000,000細胞/mLに希釈し、50μLを96ウェルの平底細胞培養プレートに播種した(Genesee Scientific;25~109)。抗DLL3pH特性改変抗体変異体、出発ABPC抗体、対照IgG1アイソタイプ対照(カタログ番号BP0297,Bioxcell)、およびビヒクル対照を、通常の培養培地中で100nMに希釈した後、300nMのZenon pHrodo iFL ヒトIgG標識試薬(ThermoFisher; Z25611)と1:1で混合した。混合物を室温で20分間インキュベートし、続いて50μLを細胞に添加した。細胞、抗DLL3抗体、およびZenon pHrodo iFL ヒトIgG標識試薬の混合物を37℃、5%CO2で24時間インキュベートした。インキュベート後、100μLの氷冷フローサイトメトリー(FC)緩衝液(リン酸緩衝食塩水(PBS)(pH7.4)+2mMのエチレンジアミン四酢酸(EDTA)+2%(v/v)の熱不活化ウシ胎児血清(HI FBS))を各ウェルに添加した。細胞を4℃にて2000rpmで2分間スピンダウンし、200μLの氷冷FC緩衝液で洗浄し、100μLの氷冷FC緩衝液中に再懸濁した。平均緑色蛍光強度は、BD Accuri C6フローサイトメトリーを使用して検出した。データを、Flowjo解析ソフトウェアを使用して解析した。非特異的RAJI(DLL3-)細胞における、抗DLL3野生型抗体(ロバルピツズマブ)および変異体の内在化およびエンドリソソーム送達を図22に示す。ロバルピツズマブおよびpH特性改変変異体(MYT1185、MYT1193およびMYT2829)は、ヒトIgG1アイソタイプ対照と同様の内在化およびエンドリソソーム送達を示し、pH特性改変が、抗DLL3結合抗体の標的依存的内在化およびエンドリソソソーム送達の特異性に影響しないことが確認された。かかるpH特性改変された抗DLL3抗体変異体であって、それらの出発ABPC抗体と比較して平均蛍光強度が2倍未満増加したものを、IgG1アイソタイプ対照と比較してさらなる解析のために選抜した(MYT1185、MYT1193、およびMYT2829)。この実験では、サンプルが読み取られている間に経時的なドリフトが観察され、これは、実験の開始および終了時にロバルピツズマブで処理された同一のサンプルを読み取ることによって補正することができた。
本発明は、その詳細な説明とともに説明されているが、上記の説明は、添付の特許請求の範囲によって定義される本発明の範囲を例示することを意図するものであり、限定するものではないことを理解されたい。他の態様、利点、および変更は、以下の特許請求の範囲の範囲内である。
>ロバルピツズマブIgGの重鎖(配列番号1)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGの軽鎖(配列番号2)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブの重鎖CDR1(配列番号3)
KASGYTFTNYGMN
>ロバルピツズマブの重鎖CDR2(配列番号4)
WINTYTGEPTYADDFKG
>ロバルピツズマブの重鎖CDR3(配列番号5)
ARIGDSSPSDY
>ロバルピツズマブの軽鎖CDR1(配列番号6)
KASQSVSNDVV
>ロバルピツズマブの軽鎖CDR2(配列番号7)
YASNRYT
>ロバルピツズマブの軽鎖CDR3(配列番号8)
QQDYTSPW
>成熟ヒトDLL3(配列番号9)
AGVFELQIHSFGPGPGPGAPRSPCSARLPCRLFFRVCLKPGLSEEAAESPCALGAALSARGPVYTEQPGAPAPDLPLPDGLLQVPFRDAWPGTFSFIIETWREELGDQIGGPAWSLLARVAGRRRLAAGGPWARDIQRAGAWELRFSYRARCEPPAVGTACTRLCRPRSAPSRCGPGLRPCAPLEDECEAPLVCRAGCSPEHGFCEQPGECRCLEGWTGPLCTVPVSTSSCLSPRGPSSATTGCLVPGPGPCDGNPCANGGSCSETPRSFECTCPRGFYGLRCEVSGVTCADGPCFNGGLCVGGADPDSAYICHCPPGFQGSNCEKRVDRCSLQPCRNGGLCLDLGHALRCRCRAGFAGPRCEHDLDDCAGRACANGGTCVEGGGAHRCSCALGFGGRDCRERADPCAARPCAHGGRCYAHFSGLVCACAPGYMGARCEFPVHPDGASALPAAPPGLRPGDPQRYLLPPALGLLVAAGVAGAALLLVHVRRRGHSQDAGSRLLAGTPEPSVHALPDALNNLRTQEGSGDGPSSSVDWNRPEDVDPQGIYVISAPSIYAREVATPLFPPLHTGRAGQRQHLLFPYPSSILSVK
>成熟ヒトDLL3(配列番号10)をコードするcDNA
GCTGGCGTCTTCGAGCTGCAGATCCACTCTTTCGGGCCGGGTCCAGGCCCTGGGGCCCCGCGGTCCCCCTGCAGCGCCCGGCTCCCCTGCCGCCTCTTCTTCAGAGTCTGCCTGAAGCCTGGGCTCTCAGAGGAGGCCGCCGAGTCCCCGTGCGCCCTGGGCGCGGCGCTGAGTGCGCGCGGACCGGTCTACACCGAGCAGCCCGGAGCGCCCGCGCCTGATCTCCCACTGCCCGACGGCCTCTTGCAGGTGCCCTTCCGGGACGCCTGGCCTGGCACCTTCTCTTTCATCATCGAAACCTGGAGAGAGGAGTTAGGAGACCAGATTGGAGGGCCCGCCTGGAGCCTGCTGGCGCGCGTGGCTGGCAGGCGGCGCTTGGCAGCCGGAGGCCCGTGGGCCCGGGACATTCAGCGCGCAGGCGCCTGGGAGCTGCGCTTCTCGTACCGCGCGCGCTGCGAGCCGCCTGCCGTCGGGACCGCGTGCACGCGCCTCTGCCGTCCGCGCAGCGCCCCCTCGCGGTGCGGTCCGGGACTGCGCCCCTGCGCACCGCTCGAGGACGAATGTGAGGCGCCGCTGGTGTGCCGAGCAGGCTGCAGCCCTGAGCATGGCTTCTGTGAACAGCCCGGTGAATGCCGATGCCTAGAGGGCTGGACTGGACCCCTCTGCACGGTCCCTGTCTCCACCAGCAGCTGCCTCAGCCCCAGGGGCCCGTCCTCTGCTACCACCGGATGCCTTGTCCCTGGGCCTGGGCCCTGTGACGGGAACCCGTGTGCCAATGGAGGCAGCTGTAGTGAGACACCCAGGTCCTTTGAATGCACCTGCCCGCGTGGGTTCTACGGGCTGCGGTGTGAGGTGAGCGGGGTGACATGTGCAGATGGACCCTGCTTCAACGGCGGCTTGTGTGTCGGGGGTGCAGACCCTGACTCTGCCTACATCTGCCACTGCCCACCCGGTTTCCAAGGCTCCAACTGTGAGAAGAGGGTGGACCGGTGCAGCCTGCAGCCATGCCGCAATGGCGGACTCTGCCTGGACCTGGGCCACGCCCTGCGCTGCCGCTGCCGCGCCGGCTTCGCGGGTCCTCGCTGCGAGCACGACCTGGACGACTGCGCGGGCCGCGCCTGCGCTAACGGCGGCACGTGTGTGGAGGGCGGCGGCGCGCACCGCTGCTCCTGCGCGCTGGGCTTCGGCGGCCGCGACTGCCGCGAGCGCGCGGACCCGTGCGCCGCGCGCCCCTGTGCTCACGGCGGCCGCTGCTACGCCCACTTCTCCGGCCTCGTCTGCGCTTGCGCTCCCGGCTACATGGGAGCGCGGTGTGAGTTCCCAGTGCACCCCGACGGCGCAAGCGCCTTGCCCGCGGCCCCGCCGGGCCTCAGGCCCGGGGACCCTCAGCGCTACCTTTTGCCTCCGGCTCTGGGACTGCTCGTGGCCGCGGGCGTGGCCGGCGCTGCGCTCTTGCTGGTCCACGTGCGCCGCCGTGGCCACTCCCAGGATGCTGGGTCTCGCTTGCTGGCTGGGACCCCGGAGCCGTCAGTCCACGCACTCCCGGATGCACTCAACAACCTAAGGACGCAGGAGGGTTCCGGGGATGGTCCGAGCTCGTCCGTAGATTGGAATCGCCCTGAAGATGTAGACCCTCAAGGGATTTATGTCATATCTGCTCCTTCCATCTACGCTCGGGAGGTAGCGACGCCCCTTTTCCCCCCGCTACACACTGGGCGCGCTGGGCAGAGGCAGCACCTGCTTTTTCCCTACCCTTCCTCGATTCTGTCCGTGAAA
>DLL3の細胞外ドメイン(配列番号11)
AGVFELQIHSFGPGPGPGAPRSPCSARLPCRLFFRVCLKPGLSEEAAESPCALGAALSARGPVYTEQPGAPAPDLPLPDGLLQVPFRDAWPGTFSFIIETWREELGDQIGGPAWSLLARVAGRRRLAAGGPWARDIQRAGAWELRFSYRARCEPPAVGTACTRLCRPRSAPSRCGPGLRPCAPLEDECEAPLVCRAGCSPEHGFCEQPGECRCLEGWTGPLCTVPVSTSSCLSPRGPSSATTGCLVPGPGPCDGNPCANGGSCSETPRSFECTCPRGFYGLRCEVSGVTCADGPCFNGGLCVGGADPDSAYICHCPPGFQGSNCEKRVDRCSLQPCRNGGLCLDLGHALRCRCRAGFAGPRCEHDLDDCAGRACANGGTCVEGGGAHRCSCALGFGGRDCRERADPCAARPCAHGGRCYAHFSGLVCACAPGYMGARCEFPVHPDGASALPAAPPGLRPGDPQRYL
>DLL3の細胞外ドメイン(配列番号12)をコードするcDNA
GCTGGCGTCTTCGAGCTGCAGATCCACTCTTTCGGGCCGGGTCCAGGCCCTGGGGCCCCGCGGTCCCCCTGCAGCGCCCGGCTCCCCTGCCGCCTCTTCTTCAGAGTCTGCCTGAAGCCTGGGCTCTCAGAGGAGGCCGCCGAGTCCCCGTGCGCCCTGGGCGCGGCGCTGAGTGCGCGCGGACCGGTCTACACCGAGCAGCCCGGAGCGCCCGCGCCTGATCTCCCACTGCCCGACGGCCTCTTGCAGGTGCCCTTCCGGGACGCCTGGCCTGGCACCTTCTCTTTCATCATCGAAACCTGGAGAGAGGAGTTAGGAGACCAGATTGGAGGGCCCGCCTGGAGCCTGCTGGCGCGCGTGGCTGGCAGGCGGCGCTTGGCAGCCGGAGGCCCGTGGGCCCGGGACATTCAGCGCGCAGGCGCCTGGGAGCTGCGCTTCTCGTACCGCGCGCGCTGCGAGCCGCCTGCCGTCGGGACCGCGTGCACGCGCCTCTGCCGTCCGCGCAGCGCCCCCTCGCGGTGCGGTCCGGGACTGCGCCCCTGCGCACCGCTCGAGGACGAATGTGAGGCGCCGCTGGTGTGCCGAGCAGGCTGCAGCCCTGAGCATGGCTTCTGTGAACAGCCCGGTGAATGCCGATGCCTAGAGGGCTGGACTGGACCCCTCTGCACGGTCCCTGTCTCCACCAGCAGCTGCCTCAGCCCCAGGGGCCCGTCCTCTGCTACCACCGGATGCCTTGTCCCTGGGCCTGGGCCCTGTGACGGGAACCCGTGTGCCAATGGAGGCAGCTGTAGTGAGACACCCAGGTCCTTTGAATGCACCTGCCCGCGTGGGTTCTACGGGCTGCGGTGTGAGGTGAGCGGGGTGACATGTGCAGATGGACCCTGCTTCAACGGCGGCTTGTGTGTCGGGGGTGCAGACCCTGACTCTGCCTACATCTGCCACTGCCCACCCGGTTTCCAAGGCTCCAACTGTGAGAAGAGGGTGGACCGGTGCAGCCTGCAGCCATGCCGCAATGGCGGACTCTGCCTGGACCTGGGCCACGCCCTGCGCTGCCGCTGCCGCGCCGGCTTCGCGGGTCCTCGCTGCGAGCACGACCTGGACGACTGCGCGGGCCGCGCCTGCGCTAACGGCGGCACGTGTGTGGAGGGCGGCGGCGCGCACCGCTGCTCCTGCGCGCTGGGCTTCGGCGGCCGCGACTGCCGCGAGCGCGCGGACCCGTGCGCCGCGCGCCCCTGTGCTCACGGCGGCCGCTGCTACGCCCACTTCTCCGGCCTCGTCTGCGCTTGCGCTCCCGGCTACATGGGAGCGCGGTGTGAGTTCCCAGTGCACCCCGACGGCGCAAGCGCCTTGCCCGCGGCCCCGCCGGGCCTCAGGCCCGGGGACCCTCAGCGCTACCTT
>ロバルピツズマブIgGヒスチジンスキャニング変異体#1の重鎖(配列番号13)
QVQLVQSGAEVKKPGASVKVSCHASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#2の重鎖(配列番号14)
QVQLVQSGAEVKKPGASVKVSCKHSGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#3の重鎖(配列番号15)
QVQLVQSGAEVKKPGASVKVSCKAHGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#4の重鎖(配列番号16)
QVQLVQSGAEVKKPGASVKVSCKASHYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#5の重鎖(配列番号17)
QVQLVQSGAEVKKPGASVKVSCKASGHTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#6の重鎖(配列番号18)
QVQLVQSGAEVKKPGASVKVSCKASGYHFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#7の重鎖(配列番号19)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#8の重鎖(配列番号20)
QVQLVQSGAEVKKPGASVKVSCKASGYTFHNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#9の重鎖(配列番号21)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTHYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#10の重鎖(配列番号22)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNHGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#11の重鎖(配列番号23)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYHMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#12の重鎖(配列番号24)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGHNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#13の重鎖(配列番号25)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMHWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#14の重鎖(配列番号26)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGHINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#15の重鎖(配列番号27)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWHNTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#16の重鎖(配列番号28)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWIHTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#17の重鎖(配列番号29)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINHYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#18の重鎖(配列番号30)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTHTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#19の重鎖(配列番号31)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYHGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#20の重鎖(配列番号32)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTHEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#21の重鎖(配列番号33)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGHPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#22の重鎖(配列番号34)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEHTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#23の重鎖(配列番号35)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPHYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#24の重鎖(配列番号36)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTHADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#25の重鎖(配列番号37)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYHDDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#26の重鎖(配列番号38)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYAHDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#27の重鎖(配列番号39)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADHFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#28の重鎖(配列番号40)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDHKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#29の重鎖(配列番号41)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFHGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#30の重鎖(配列番号42)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKHRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#31の重鎖(配列番号43)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCHRIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#32の重鎖(配列番号44)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCAHIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#33の重鎖(配列番号45)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARHGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#34の重鎖(配列番号46)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIHDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#35の重鎖(配列番号47)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGHSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#36の重鎖(配列番号48)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDHSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#37の重鎖(配列番号49)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSHPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#38の重鎖(配列番号50)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSHSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#39の重鎖(配列番号51)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPHDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#40の重鎖(配列番号52)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSHYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#41の重鎖(配列番号53)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDHWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#1の軽鎖(配列番号54)
EIVMTQSPATLSVSPGERATLSCHASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#2の軽鎖(配列番号55)
EIVMTQSPATLSVSPGERATLSCKHSQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#3の軽鎖(配列番号56)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#4の軽鎖(配列番号57)
EIVMTQSPATLSVSPGERATLSCKASHSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#5の軽鎖(配列番号58)
EIVMTQSPATLSVSPGERATLSCKASQHVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#6の軽鎖(配列番号59)
EIVMTQSPATLSVSPGERATLSCKASQSHSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#7の軽鎖(配列番号60)
EIVMTQSPATLSVSPGERATLSCKASQSVHNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#8の軽鎖(配列番号61)
EIVMTQSPATLSVSPGERATLSCKASQSVSHDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#9の軽鎖(配列番号62)
EIVMTQSPATLSVSPGERATLSCKASQSVSNHVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#10の軽鎖(配列番号63)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDHVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#11の軽鎖(配列番号64)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVHWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#12の軽鎖(配列番号65)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#13の軽鎖(配列番号66)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYHSNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#14の軽鎖(配列番号67)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYAHNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#15の軽鎖(配列番号68)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASHRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#16の軽鎖(配列番号69)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNHYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#17の軽鎖(配列番号70)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRHTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#18の軽鎖(配列番号71)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYHGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#19の軽鎖(配列番号72)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCHQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#20の軽鎖(配列番号73)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQHDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#21の軽鎖(配列番号74)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQHYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#22の軽鎖(配列番号75)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDHTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#23の軽鎖(配列番号76)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#24の軽鎖(配列番号77)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTHPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#25の軽鎖(配列番号78)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSHWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#26の軽鎖(配列番号79)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPHTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#27の軽鎖(配列番号80)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWHFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#1の重鎖組み合わせ(配列番号81)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTNYGMNWVRQAPGQGLEWMGWINTHTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#2の重鎖組み合わせ(配列番号82)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTHYGMNWVRQAPGQGLEWMGWINTHTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#3の重鎖組み合わせ(配列番号83)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTHYGMNWVRQAPGQGLEWMGWINTYHGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#4の重鎖組み合わせ(配列番号84)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTHYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPHDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#5の重鎖組み合わせ(配列番号85)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTHHGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#6の重鎖組み合わせ(配列番号86)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTHTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPHDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#7の重鎖組み合わせ(配列番号87)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTHYGMNWVRQAPGQGLEWMGWINTHTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#8の重鎖組み合わせ(配列番号88)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTHYGMNWVRQAPGQGLEWMGWINTHHGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#9の重鎖組み合わせ(配列番号89)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTHYGMNWVRQAPGQGLEWMGWINTHTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPHDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#10の重鎖組み合わせ(配列番号90)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTHYGMNWVRQAPGQGLEWMGWINTYHGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPHDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#11の重鎖組み合わせ(配列番号91)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTHHGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPHDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#12の重鎖組み合わせ(配列番号92)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTHYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#13の重鎖組み合わせ(配列番号93)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTNYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPHDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#14の重鎖組み合わせ(配列番号94)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQGLEWMGWINTYHGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPHDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#15の重鎖組み合わせ(配列番号95)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTHYGMNWVRQAPGQGLEWMGWINTYHGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#16の重鎖組み合わせ(配列番号96)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTHYGMNWVRQAPGQGLEWMGWINTYTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPHDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#17の重鎖組み合わせ(配列番号97)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTNYGMNWVRQAPGQGLEWMGWINTHHGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPSDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#18の重鎖組み合わせ(配列番号98)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTNYGMNWVRQAPGQGLEWMGWINTHTGEPTYADDFKGRVTMTTDTSTSTAYMELRSLRSDDTAVYYCARIGDSSPHDYWGQGTLVTVSS
>ロバルピツズマブIgGヒスチジンスキャニング変異体#1の軽鎖組み合わせ(配列番号99)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#2の軽鎖組み合わせ(配列番号100)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#3の軽鎖組み合わせ(配列番号101)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTHPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#4の軽鎖組み合わせ(配列番号102)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWHFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#5の軽鎖組み合わせ(配列番号103)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#6の軽鎖組み合わせ(配列番号104)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTHPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#7の軽鎖組み合わせ(配列番号105)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWHFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#8の軽鎖組み合わせ(配列番号106)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHHPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#9の軽鎖組み合わせ(配列番号107)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHSPWHFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#10の軽鎖組み合わせ(配列番号108)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTHPWHFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#11の軽鎖組み合わせ(配列番号109)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHSPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#12の軽鎖組み合わせ(配列番号110)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTHPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#13の軽鎖組み合わせ(配列番号111)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTSPWHFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#14の軽鎖組み合わせ(配列番号112)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHHPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#15の軽鎖組み合わせ(配列番号113)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHSPWHFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#16の軽鎖組み合わせ(配列番号114)
EIVMTQSPATLSVSPGERATLSCKAHQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTHPWHFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#17の軽鎖組み合わせ(配列番号115)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHHPWTFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#18の軽鎖組み合わせ(配列番号116)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHSPWHFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#19の軽鎖組み合わせ(配列番号117)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYHASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYTHPWHFGQGTKLEIK
>ロバルピツズマブIgGヒスチジンスキャニング変異体#20の軽鎖組み合わせ(配列番号118)
EIVMTQSPATLSVSPGERATLSCKASQSVSNDVVWYQQKPGQAPRLLIYYASNRYTGIPARFSGSGSGTEFTLTISSLQSEDFAVYYCQQDYHHPWHFGQGTKLEIK
>SC16.4IgG(配列番号119)の重鎖
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgG(配列番号120)の軽鎖
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#1の重鎖(配列番号121)
QIQLVQSGPELKKPGETVKISCKASHYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#2の重鎖(配列番号122)
QIQLVQSGPELKKPGETVKISCKASGHTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#3の重鎖(配列番号123)
QIQLVQSGPELKKPGETVKISCKASGYHFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#4の重鎖(配列番号124)
QIQLVQSGPELKKPGETVKISCKASGYTHTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#5の重鎖(配列番号125)
QIQLVQSGPELKKPGETVKISCKASGYTFHDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#6の重鎖(配列番号126)
QIQLVQSGPELKKPGETVKISCKASGYTFTHYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#7の重鎖(配列番号127)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#8の重鎖(配列番号128)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYHMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#9の重鎖(配列番号129)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSHHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#10の重鎖(配列番号130)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMAWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#11の重鎖(配列番号131)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGHINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#12の重鎖(配列番号132)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWHNTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#13の重鎖(配列番号133)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWIHTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#14の重鎖(配列番号134)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINHETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#15の重鎖(配列番号135)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTHTGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#16の重鎖(配列番号136)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTEHGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#17の重鎖(配列番号137)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETHEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#18の重鎖(配列番号138)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#19の重鎖(配列番号139)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEHGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#20の重鎖(配列番号140)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPHYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#21の重鎖(配列番号141)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGHADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#22の重鎖(配列番号142)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYHDDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#23の重鎖(配列番号143)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#24の重鎖(配列番号144)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADHFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#25の重鎖(配列番号145)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDHKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#26の重鎖(配列番号146)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFHGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#27の重鎖(配列番号147)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKHRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#28の重鎖(配列番号148)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCHRYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#29の重鎖(配列番号149)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCAHYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#30の重鎖(配列番号150)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#31の重鎖(配列番号151)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#32の重鎖(配列番号152)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDHYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#33の重鎖(配列番号153)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGHAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#34の重鎖(配列番号154)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYHMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#35の重鎖(配列番号155)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAHDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#36の重鎖(配列番号156)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#37の重鎖(配列番号157)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDHWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#1の軽鎖(配列番号158)
DIQMTQTTSSLSASLGDRVTISCHASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#2の軽鎖(配列番号159)
DIQMTQTTSSLSASLGDRVTISCRHSQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#3の軽鎖(配列番号160)
DIQMTQTTSSLSASLGDRVTISCRAHQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#4の軽鎖(配列番号161)
DIQMTQTTSSLSASLGDRVTISCRASHDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#5の軽鎖(配列番号162)
DIQMTQTTSSLSASLGDRVTISCRASQHISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#6の軽鎖(配列番号163)
DIQMTQTTSSLSASLGDRVTISCRASQDHSNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#7の軽鎖(配列番号164)
DIQMTQTTSSLSASLGDRVTISCRASQDIHNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#8の軽鎖(配列番号165)
DIQMTQTTSSLSASLGDRVTISCRASQDISHYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#9の軽鎖(配列番号166)
DIQMTQTTSSLSASLGDRVTISCRASQDISNHLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#10の軽鎖(配列番号167)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYHNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#11の軽鎖(配列番号168)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLHWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#12の軽鎖(配列番号169)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYHSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#13の軽鎖(配列番号170)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTHRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#14の軽鎖(配列番号171)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSHLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#15の軽鎖(配列番号172)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRHHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#16の軽鎖(配列番号173)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLASGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#17の軽鎖(配列番号174)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHHGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#18の軽鎖(配列番号175)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCHQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#19の軽鎖(配列番号176)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQHGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#20の軽鎖(配列番号177)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQHDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#21の軽鎖(配列番号178)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGHMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#22の軽鎖(配列番号179)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDHLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#23の軽鎖(配列番号180)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMHPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#24の軽鎖(配列番号181)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLHWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#25の軽鎖(配列番号182)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPHTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#26の軽鎖(配列番号183)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWHFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#27の軽鎖(配列番号184)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLNWYQQKPDGTVKLLIYHTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#1の重鎖組み合わせ(配列番号185)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#2の重鎖組み合わせ(配列番号186)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#3の重鎖組み合わせ(配列番号187)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#4の重鎖組み合わせ(配列番号188)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#5の重鎖組み合わせ(配列番号189)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#6の重鎖組み合わせ(配列番号190)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#7の重鎖組み合わせ(配列番号191)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#8の重鎖組み合わせ(配列番号192)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#9の重鎖組み合わせ(配列番号193)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#10の重鎖組み合わせ(配列番号194)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#11の重鎖組み合わせ(配列番号195)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGHPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#12の重鎖組み合わせ(配列番号196)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#13の重鎖組み合わせ(配列番号197)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#14の重鎖組み合わせ(配列番号198)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#15の重鎖組み合わせ(配列番号199)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#16の重鎖組み合わせ(配列番号200)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#17の重鎖組み合わせ(配列番号201)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#18の重鎖組み合わせ(配列番号202)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#19の重鎖組み合わせ(配列番号203)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#20の重鎖組み合わせ(配列番号204)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#21の重鎖組み合わせ(配列番号205)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGHPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#22の重鎖組み合わせ(配列番号206)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGHPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#23の重鎖組み合わせ(配列番号207)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#24の重鎖組み合わせ(配列番号208)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#25の重鎖組み合わせ(配列番号209)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#26の重鎖組み合わせ(配列番号210)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGHPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHDGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#27の重鎖組み合わせ(配列番号211)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#28の重鎖組み合わせ(配列番号212)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#29の重鎖組み合わせ(配列番号213)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#30の重鎖組み合わせ(配列番号214)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#31の重鎖組み合わせ(配列番号215)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#32の重鎖組み合わせ(配列番号216)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#33の重鎖組み合わせ(配列番号217)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#34の重鎖組み合わせ(配列番号218)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#35の重鎖組み合わせ(配列番号219)
QIQLVQSGPELKKPGETVKISCKASGYTFTDHSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#36の重鎖組み合わせ(配列番号220)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#37の重鎖組み合わせ(配列番号221)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#38の重鎖組み合わせ(配列番号222)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGHPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#39の重鎖組み合わせ(配列番号223)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHHGYAMDYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#40の重鎖組み合わせ(配列番号224)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYAHDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARYHGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#41の重鎖組み合わせ(配列番号225)
QIQLVQSGPELKKPGETVKISCKASGYTFTDYSMHWVKQAPGKGLKWMGWINTETGEPGYADDFKGRFAFSLETSASTAYLQINNLKNEDTATYFCARHHGYAMHYWGQGTSVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#1の軽鎖組み合わせ(配列番号226)
DIQMTQTTSSLSASLGDRVTISCRASQDHSNHLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#2の軽鎖組み合わせ(配列番号227)
DIQMTQTTSSLSASLGDRVTISCRASQDHSNYLHWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#3の軽鎖組み合わせ(配列番号228)
DIQMTQTTSSLSASLGDRVTISCRASQDHSNYLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDHLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#4の軽鎖組み合わせ(配列番号229)
DIQMTQTTSSLSASLGDRVTISCRASQDISNHLHWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#5の軽鎖組み合わせ(配列番号230)
DIQMTQTTSSLSASLGDRVTISCRASQDISNHLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDHLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#6の軽鎖組み合わせ(配列番号231)
DIQMTQTTSSLSASLGDRVTISCRASQDISNYLHWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDHLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#7の軽鎖組み合わせ(配列番号232)
DIQMTQTTSSLSASLGDRVTISCRASQDHSNHLHWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDMLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#8の軽鎖組み合わせ(配列番号233)
DIQMTQTTSSLSASLGDRVTISCRASQDHSNHLNWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDHLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#9の軽鎖組み合わせ(配列番号234)
DIQMTQTTSSLSASLGDRVTISCRASQDHSNYLHWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDHLPWTFGGGTKLEIK
>SC16.4IgGヒスチジンスキャニング変異体#10の軽鎖組み合わせ(配列番号235)
DIQMTQTTSSLSASLGDRVTISCRASQDISNHLHWYQQKPDGTVKLLIYYTSRLHSGVPSRFSGSGSGTDYSLTISNLELEDIATYFCQQGDHLPWTFGGGTKLEIK
>hSC16.13IgG(配列番号236)の重鎖
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgG(配列番号237)の軽鎖
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#1の重鎖(配列番号238)
QITLKESGPTLVKPTQTLTLTCTFSHFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#2の重鎖(配列番号239)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#3の重鎖(配列番号240)
QITLKESGPTLVKPTQTLTLTCTFSGFHLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#4の重鎖(配列番号241)
QITLKESGPTLVKPTQTLTLTCTFSGFSHSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#5の重鎖(配列番号242)
QITLKESGPTLVKPTQTLTLTCTFSGFSLHTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#6の重鎖(配列番号243)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSHSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#7の重鎖(配列番号244)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTHGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#8の重鎖(配列番号245)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSHMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#9の重鎖(配列番号246)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGHGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#10の重鎖(配列番号247)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMHVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#11の重鎖(配列番号248)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGHGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#12の重鎖(配列番号249)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVHWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#13の重鎖(配列番号250)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAAIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#14の重鎖(配列番号251)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHHWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#15の重鎖(配列番号252)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIHWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#16の重鎖(配列番号253)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#17の重鎖(配列番号254)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWHDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#18の重鎖(配列番号255)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDHVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#19の重鎖(配列番号256)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDHKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#20の重鎖(配列番号257)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVHRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#21の重鎖(配列番号258)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKHYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#22の重鎖(配列番号259)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRHSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#23の重鎖(配列番号260)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYHPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#24の重鎖(配列番号261)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSHSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#25の重鎖(配列番号262)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPHLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#26の重鎖(配列番号263)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSHKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#27の重鎖(配列番号264)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLHSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#28の重鎖(配列番号265)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKHRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#29の重鎖(配列番号266)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCHRIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#30の重鎖(配列番号267)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCAHIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#31の重鎖(配列番号268)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARHVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#32の重鎖(配列番号269)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIHSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#33の重鎖(配列番号270)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#34の重鎖(配列番号271)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSHDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#35の重鎖(配列番号272)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFHNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#36の重鎖(配列番号273)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDHDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#37の重鎖(配列番号274)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#38の重鎖(配列番号275)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDHVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#39の重鎖(配列番号276)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVHSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#40の重鎖(配列番号277)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVHAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#41の重鎖(配列番号278)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSHMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#42の重鎖(配列番号279)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAHDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#43の重鎖(配列番号280)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMHYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#44の重鎖(配列番号281)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDHWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#1の軽鎖(配列番号282)
DIQMTQSPSSLSASVGDRVTITCHASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#2の軽鎖(配列番号283)
DIQMTQSPSSLSASVGDRVTITCSHSSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#3の軽鎖(配列番号284)
DIQMTQSPSSLSASVGDRVTITCSAHSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#4の軽鎖(配列番号285)
DIQMTQSPSSLSASVGDRVTITCSASHSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#5の軽鎖(配列番号286)
DIQMTQSPSSLSASVGDRVTITCSASSHVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#6の軽鎖(配列番号287)
DIQMTQSPSSLSASVGDRVTITCSASSSHSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#7の軽鎖(配列番号288)
DIQMTQSPSSLSASVGDRVTITCSASSSVHYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#8の軽鎖(配列番号289)
DIQMTQSPSSLSASVGDRVTITCSASSSVSHMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#9の軽鎖(配列番号290)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYHYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#10の軽鎖(配列番号291)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMHWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#11の軽鎖(配列番号292)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYHTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#12の軽鎖(配列番号293)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLHSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#13の軽鎖(配列番号294)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTHNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#14の軽鎖(配列番号295)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSHLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#15の軽鎖(配列番号296)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNHASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#16の軽鎖(配列番号297)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLHSGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#17の軽鎖(配列番号298)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLAHGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#18の軽鎖(配列番号299)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCHQWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#19の軽鎖(配列番号300)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQHWRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#20の軽鎖(配列番号301)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQHRSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#21の軽鎖(配列番号302)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWHSNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#22の軽鎖(配列番号303)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRHNPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#23の軽鎖(配列番号304)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSHPFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#24の軽鎖(配列番号305)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNHFTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#25の軽鎖(配列番号306)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPHTFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#26の軽鎖(配列番号307)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMYWYQQKPGKAPKLLIYLTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFHFGQGTKLEIK
>hSC16.13IgGヒスチジンスキャニング変異体#1の重鎖組み合わせ(配列番号308)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAAIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#2の重鎖組み合わせ(配列番号309)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAHIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#3の重鎖組み合わせ(配列番号310)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#4の重鎖組み合わせ(配列番号311)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#5の重鎖組み合わせ(配列番号312)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAAIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#6の重鎖組み合わせ(配列番号313)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAAIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#7の重鎖組み合わせ(配列番号314)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAAIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#8の重鎖組み合わせ(配列番号315)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#9の重鎖組み合わせ(配列番号316)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#10の重鎖組み合わせ(配列番号317)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#11の重鎖組み合わせ(配列番号318)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAAIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#12の重鎖組み合わせ(配列番号319)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAAIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#13の重鎖組み合わせ(配列番号320)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAAIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#14の重鎖組み合わせ(配列番号321)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAHIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#15の重鎖組み合わせ(配列番号322)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAHIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#16の重鎖組み合わせ(配列番号323)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAHIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#17の重鎖組み合わせ(配列番号324)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAAIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#18の重鎖組み合わせ(配列番号325)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAAIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#19の重鎖組み合わせ(配列番号326)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAAIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#20の重鎖組み合わせ(配列番号327)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAHIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#21の重鎖組み合わせ(配列番号328)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAAIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNDVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#22の重鎖組み合わせ(配列番号329)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAAIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVSFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#23の重鎖組み合わせ(配列番号330)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAAIWWDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#24の重鎖組み合わせ(配列番号331)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAHIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#25の重鎖組み合わせ(配列番号332)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLAAIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNHVVSAMDYWGQGTLVTVSS
>hSC16.13IgGヒスチジンスキャニング変異体#26の重鎖組み合わせ(配列番号333)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLAAIWHDDVKRYSPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARIVHFDNHVVSAMDYWGQGTLVTVSS
>SC16.4IgGヒスチジンスキャニング変異体#1の軽鎖組み合わせ(配列番号334)
DIQMTQSPSSLSASVGDRVTITCSASSSVSYMHWYQQKPGKAPKLLIYHTSNLASGVPSRFSGSGSGTDFTLTISSLQPEDFATYYCQQWRSNPFTFGQGTKLEIK
>hSC16.15IgG(配列番号335)の重鎖
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgG(配列番号336)の軽鎖
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#1の重鎖(配列番号337)
QVQLVQSGAEVKKPGASVKVSCHASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#2の重鎖(配列番号338)
QVQLVQSGAEVKKPGASVKVSCKHSGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#3の重鎖(配列番号339)
QVQLVQSGAEVKKPGASVKVSCKAHGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#4の重鎖(配列番号340)
QVQLVQSGAEVKKPGASVKVSCKASHYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#5の重鎖(配列番号341)
QVQLVQSGAEVKKPGASVKVSCKASGHTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#6の重鎖(配列番号342)
QVQLVQSGAEVKKPGASVKVSCKASGYHFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#7の重鎖(配列番号343)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#8の重鎖(配列番号344)
QVQLVQSGAEVKKPGASVKVSCKASGYTFHRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#9の重鎖(配列番号345)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTHYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#10の重鎖(配列番号346)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRHWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#11の重鎖(配列番号347)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYHIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#12の重鎖(配列番号348)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWHHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#13の重鎖(配列番号349)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIAWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#14の重鎖(配列番号350)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGHINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#15の重鎖(配列番号351)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYHNPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#16の重鎖(配列番号352)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYIHPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#17の重鎖(配列番号353)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINHTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#18の重鎖(配列番号354)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPHTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#19の重鎖(配列番号355)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTHVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#20の重鎖(配列番号356)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTHYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#21の重鎖(配列番号357)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVHTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#22の重鎖(配列番号358)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYHEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#23の重鎖(配列番号359)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTHFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#24の重鎖(配列番号360)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEHNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#25の重鎖(配列番号361)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFHQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#26の重鎖(配列番号362)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNHNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#27の重鎖(配列番号363)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQHFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#28の重鎖(配列番号364)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNHKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#29の重鎖(配列番号365)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFHDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#30の重鎖(配列番号366)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKHRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#31の重鎖(配列番号367)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCHRGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#32の重鎖(配列番号368)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCAHGGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#33の重鎖(配列番号369)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARHGSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#34の重鎖(配列番号370)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGHSNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#35の重鎖(配列番号371)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGHNFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#36の重鎖(配列番号372)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSHFFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#37の重鎖(配列番号373)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNHFDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#38の重鎖(配列番号374)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFHDYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#39の重鎖(配列番号375)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFHYWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#40の重鎖(配列番号376)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTRYWIHWIRQAPGQGLEWMGYINPTTVYTEFNQNFKDRVTMTRDTSTSTVYMELSSLRSEDTAVYYCARGGSNFFDHWGQGTTVTVSS
>hSC16.15IgGヒスチジンスキャニング変異体#1の軽鎖(配列番号377)
AIQLTQSPSSLSASVGDRVTITCRASHNIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#2の軽鎖(配列番号378)
AIQLTQSPSSLSASVGDRVTITCRASEHIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#3の軽鎖(配列番号379)
AIQLTQSPSSLSASVGDRVTITCRASENHYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#4の軽鎖(配列番号380)
AIQLTQSPSSLSASVGDRVTITCRASENIHYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#5の軽鎖(配列番号381)
AIQLTQSPSSLSASVGDRVTITCRASENIYHNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#6の軽鎖(配列番号382)
AIQLTQSPSSLSASVGDRVTITCRASENIYYHLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#7の軽鎖(配列番号383)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNHAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#8の軽鎖(配列番号384)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLHWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#9の軽鎖(配列番号385)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYHANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#10の軽鎖(配列番号386)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTHNSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#11の軽鎖(配列番号387)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTAHSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#12の軽鎖(配列番号388)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANHLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#13の軽鎖(配列番号389)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSHEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#14の軽鎖(配列番号390)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLHDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#15の軽鎖(配列番号391)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEHGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#16の軽鎖(配列番号392)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCHQAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#17の軽鎖(配列番号393)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKHAYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#18の軽鎖(配列番号394)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQHYDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#19の軽鎖(配列番号395)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAHDVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#20の軽鎖(配列番号396)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYHVPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#21の軽鎖(配列番号397)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDHPPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#22の軽鎖(配列番号398)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVHPTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#23の軽鎖(配列番号399)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPHTFGGGTKLEIK
>hSC16.15IgGヒスチジンスキャニング変異体#24の軽鎖(配列番号400)
AIQLTQSPSSLSASVGDRVTITCRASENIYYNLAWYQQKPGKAPKLLIYTANSLEDGVPSRFSGSGSGTDFTLTISSLQPEDFATYFCKQAYDVPPHFGGGTKLEIK
>hSC16.25IgG(配列番号401)の重鎖
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgG(配列番号402)の軽鎖
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#1の重鎖(配列番号403)
QITLKESGPTLVKPTQTLTLTCTFSHFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#2の重鎖(配列番号404)
QITLKESGPTLVKPTQTLTLTCTFSGHSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#3の重鎖(配列番号405)
QITLKESGPTLVKPTQTLTLTCTFSGFHLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#4の重鎖(配列番号406)
QITLKESGPTLVKPTQTLTLTCTFSGFSHSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#5の重鎖(配列番号407)
QITLKESGPTLVKPTQTLTLTCTFSGFSLHTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#6の重鎖(配列番号408)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSHSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#7の重鎖(配列番号409)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTHGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#8の重鎖(配列番号410)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSHMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#9の重鎖(配列番号411)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGHGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#10の重鎖(配列番号412)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMHVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#11の重鎖(配列番号413)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGHGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#12の重鎖(配列番号414)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVHWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#13の重鎖(配列番号415)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTHIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#14の重鎖(配列番号416)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDHWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#15の重鎖(配列番号417)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIHWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#16の重鎖(配列番号418)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWHDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#17の重鎖(配列番号419)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWHDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#18の重鎖(配列番号420)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDHNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#19の重鎖(配列番号421)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDHKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#20の重鎖(配列番号422)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNHYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#21の重鎖(配列番号423)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKHYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#22の重鎖(配列番号424)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYHNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#23の重鎖(配列番号425)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYHPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#24の重鎖(配列番号426)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNHSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#25の重鎖(配列番号427)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPHLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#26の重鎖(配列番号428)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSHKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#27の重鎖(配列番号429)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLHSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#28の重鎖(配列番号430)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKHRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#29の重鎖(配列番号431)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCHRRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#30の重鎖(配列番号432)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCAHRVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#31の重鎖(配列番号433)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARHVNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#32の重鎖(配列番号434)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRHNYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#33の重鎖(配列番号435)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVHYYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#34の重鎖(配列番号436)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNHYYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#35の重鎖(配列番号437)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYHYDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#36の重鎖(配列番号438)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYHDPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#37の重鎖(配列番号439)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYHPYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#38の重鎖(配列番号440)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDHYYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#39の重鎖(配列番号441)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPHYAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#40の重鎖(配列番号442)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYHAMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#41の重鎖(配列番号443)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYHMDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#42の重鎖(配列番号444)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAHDYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#43の重鎖(配列番号445)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMHYWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#44の重鎖(配列番号446)
QITLKESGPTLVKPTQTLTLTCTFSGFSLSTSGMGVGWIRQPPGKALEWLTDIWWDDNKYYNPSLKSRLTITKDTSKNQVVLTMTNMDPVDTATYYCARRVNYYYDPYYAMDHWGQGTTLVTVSS
>hSC16.25IgGヒスチジンスキャニング変異体#1の軽鎖(配列番号447)
EIVLTQSPDFQSVTPKEKVTITCSASHSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#2の軽鎖(配列番号448)
EIVLTQSPDFQSVTPKEKVTITCSASSHVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#3の軽鎖(配列番号449)
EIVLTQSPDFQSVTPKEKVTITCSASSSHSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#4の軽鎖(配列番号450)
EIVLTQSPDFQSVTPKEKVTITCSASSSVHYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#5の軽鎖(配列番号451)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSHMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#6の軽鎖(配列番号452)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYHHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#7の軽鎖(配列番号453)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMAWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#8の軽鎖(配列番号454)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKHSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#9の軽鎖(配列番号455)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDHSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#10の軽鎖(配列番号456)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSHKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#11の軽鎖(配列番号457)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSHLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#12の軽鎖(配列番号458)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKHASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#13の軽鎖(配列番号459)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLHSGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#14の軽鎖(配列番号460)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLAHGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#15の軽鎖(配列番号461)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCHQWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#16の軽鎖(配列番号462)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQHWSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#17の軽鎖(配列番号463)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQHSSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#18の軽鎖(配列番号464)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWHSNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#19の軽鎖(配列番号465)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSHNPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#20の軽鎖(配列番号466)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSHPLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#21の軽鎖(配列番号467)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNHLTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#22の軽鎖(配列番号468)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPHTFGQGTKLEIK
>hSC16.25IgGヒスチジンスキャニング変異体#23の軽鎖(配列番号469)
EIVLTQSPDFQSVTPKEKVTITCSASSSVSYMHWYQQKPDQSPKLLIKDSSKLASGVPSRFSGSGSGTDFTLTINSLEAEDAATYYCQQWSSNPLHFGQGTKLEIK
>hSC16.34IgG(配列番号470)の重鎖
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgG(配列番号471)の軽鎖
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#1の重鎖(配列番号472)
QVQLVQSGAEVKKPGASVKVSCHASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#2の重鎖(配列番号473)
QVQLVQSGAEVKKPGASVKVSCKHSGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#3の重鎖(配列番号474)
QVQLVQSGAEVKKPGASVKVSCKAHGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#4の重鎖(配列番号475)
QVQLVQSGAEVKKPGASVKVSCKASHYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#5の重鎖(配列番号476)
QVQLVQSGAEVKKPGASVKVSCKASGHTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#6の重鎖(配列番号477)
QVQLVQSGAEVKKPGASVKVSCKASGYHFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#7の重鎖(配列番号478)
QVQLVQSGAEVKKPGASVKVSCKASGYTHTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#8の重鎖(配列番号479)
QVQLVQSGAEVKKPGASVKVSCKASGYTFHNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#9の重鎖(配列番号480)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTHYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#10の重鎖(配列番号481)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNHGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#11の重鎖(配列番号482)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYHMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#12の重鎖(配列番号483)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGHNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#13の重鎖(配列番号484)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMHWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#14の重鎖(配列番号485)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGHINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#15の重鎖(配列番号486)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWHNTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#16の重鎖(配列番号487)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWIHTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#17の重鎖(配列番号488)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINHYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#18の重鎖(配列番号489)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTHTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#19の重鎖(配列番号490)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYHGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#20の重鎖(配列番号491)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTHDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#21の重鎖(配列番号492)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGHPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#22の重鎖(配列番号493)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDHTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#23の重鎖(配列番号494)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPHYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#24の重鎖(配列番号495)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTHADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#25の重鎖(配列番号496)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYHDDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#26の重鎖(配列番号497)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYAHDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#27の重鎖(配列番号498)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADHFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#28の重鎖(配列番号499)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDHKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#29の重鎖(配列番号500)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFHGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#30の重鎖(配列番号501)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKHRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#31の重鎖(配列番号502)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCHRIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#32の重鎖(配列番号503)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCAHIGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#33の重鎖(配列番号504)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARHGGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#34の重鎖(配列番号505)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIHGNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#35の重鎖(配列番号506)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGHNSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#36の重鎖(配列番号507)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGHSPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#37の重鎖(配列番号508)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNHPSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#38の重鎖(配列番号509)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSHSDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#39の重鎖(配列番号510)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPHDYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#40の重鎖(配列番号511)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSHYWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#41の重鎖(配列番号512)
QVQLVQSGAEVKKPGASVKVSCKASGYTFTNYGMNWVRQAPGQRLEWMGWINTYTGDPTYADDFKGRVTITRDTSASTAYMELSSLRSEDTAVYYCARIGGNSPSDHWGQGTTVTVSS
>hSC16.34IgGヒスチジンスキャニング変異体#1の軽鎖(配列番号513)
DIQMTQSPSSLSASVGDRVTITCKASHSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#2の軽鎖(配列番号514)
DIQMTQSPSSLSASVGDRVTITCKASQHVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#3の軽鎖(配列番号515)
DIQMTQSPSSLSASVGDRVTITCKASQSHSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#4の軽鎖(配列番号516)
DIQMTQSPSSLSASVGDRVTITCKASQSVHNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#5の軽鎖(配列番号517)
DIQMTQSPSSLSASVGDRVTITCKASQSVSHDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#6の軽鎖(配列番号518)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNHVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#7の軽鎖(配列番号519)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDHAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#8の軽鎖(配列番号520)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVHWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#9の軽鎖(配列番号521)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYHASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#10の軽鎖(配列番号522)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYHSNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#11の軽鎖(配列番号523)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYAHNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#12の軽鎖(配列番号524)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASHRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#13の軽鎖(配列番号525)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNHYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#14の軽鎖(配列番号526)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRHSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#15の軽鎖(配列番号527)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYHGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#16の軽鎖(配列番号528)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCHQDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#17の軽鎖(配列番号529)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQHDYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#18の軽鎖(配列番号530)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQHYSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#19の軽鎖(配列番号531)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDHSSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#20の軽鎖(配列番号532)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYHSPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#21の軽鎖(配列番号533)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSHPWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#22の軽鎖(配列番号534)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSHWTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#23の軽鎖(配列番号535)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPHTFGGGTKVEIK
>hSC16.34IgGヒスチジンスキャニング変異体#24の軽鎖(配列番号536)
DIQMTQSPSSLSASVGDRVTITCKASQSVSNDVAWYQQKPGKVPKLLIYYASNRYSGVPSRFSGSGSGTDFTLTISSLQPEDVATYFCQQDYSSPWHFGGGTKVEIK
>SC16.67IgG(配列番号537)の重鎖
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgG(配列番号538)の軽鎖
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#1の重鎖(配列番号539)
EVQLVETGGGLVQPKGSLKLSCAVSHFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#2の重鎖(配列番号540)
EVQLVETGGGLVQPKGSLKLSCAVSAHTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#3の重鎖(配列番号541)
EVQLVETGGGLVQPKGSLKLSCAVSAFHFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#4の重鎖(配列番号542)
EVQLVETGGGLVQPKGSLKLSCAVSAFTHTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#5の重鎖(配列番号543)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFHTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#6の重鎖(配列番号544)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTHYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#7の重鎖(配列番号545)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTHAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#8の重鎖(配列番号546)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYHMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#9の重鎖(配列番号547)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAHNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#10の重鎖(配列番号548)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMHWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#11の重鎖(配列番号549)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVAHIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#12の重鎖(配列番号550)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARHRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#13の重鎖(配列番号551)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIHNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#14の重鎖(配列番号552)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRHKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#15の重鎖(配列番号553)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNHSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#16の重鎖(配列番号554)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKHNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#17の重鎖(配列番号555)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSHNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#18の重鎖(配列番号556)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNHYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#19の重鎖(配列番号557)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNHATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#20の重鎖(配列番号558)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYHTYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#21の重鎖(配列番号559)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYAHYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#22の重鎖(配列番号560)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATHYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#23の重鎖(配列番号561)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYHADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#24の重鎖(配列番号562)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYHDSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#25の重鎖(配列番号563)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYAHSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#26の重鎖(配列番号564)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADHVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#27の重鎖(配列番号565)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSHKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#28の重鎖(配列番号566)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVHDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#29の重鎖(配列番号567)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKHRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#30の重鎖(配列番号568)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCHFYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#31の重鎖(配列番号569)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVHYYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#32の重鎖(配列番号570)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFHYDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#33の重鎖(配列番号571)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYHDYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#34の重鎖(配列番号572)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYHYVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#35の重鎖(配列番号573)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDHVYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#36の重鎖(配列番号574)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYHYWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#37の重鎖(配列番号575)
EVQLVETGGGLVQPKGSLKLSCAVSAFTFTTYAMNWVRQAPGKGLEWVARIRNKSNNYATYYADSVKDRFTISRDDSQSMLYLQMNNLKIEDTAMYYCVFYYDYVHWGQGTLVTVSA
>SC16.67IgGヒスチジンスキャニング変異体#1の軽鎖(配列番号576)
QAVVTQESALTTSPGETVTLTCHSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#2の軽鎖(配列番号577)
QAVVTQESALTTSPGETVTLTCRHSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#3の軽鎖(配列番号578)
QAVVTQESALTTSPGETVTLTCRSHTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#4の軽鎖(配列番号579)
QAVVTQESALTTSPGETVTLTCRSSHGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#5の軽鎖(配列番号580)
QAVVTQESALTTSPGETVTLTCRSSTHAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#6の軽鎖(配列番号581)
QAVVTQESALTTSPGETVTLTCRSSTGHVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#7の軽鎖(配列番号582)
QAVVTQESALTTSPGETVTLTCRSSTGAHTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#8の軽鎖(配列番号583)
QAVVTQESALTTSPGETVTLTCRSSTGAVHTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#9の軽鎖(配列番号584)
QAVVTQESALTTSPGETVTLTCRSSTGAVTHSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#10の軽鎖(配列番号585)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTHNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#11の軽鎖(配列番号586)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSHYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#12の軽鎖(配列番号587)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNHANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#13の軽鎖(配列番号588)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYHNWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#14の軽鎖(配列番号589)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYAHWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#15の軽鎖(配列番号590)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGHTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#16の軽鎖(配列番号591)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGHNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#17の軽鎖(配列番号592)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTHNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#18の軽鎖(配列番号593)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNHRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#19の軽鎖(配列番号594)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNHAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#20の軽鎖(配列番号595)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRHPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#21の軽鎖(配列番号596)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAHGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#22の軽鎖(配列番号597)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCHLWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#23の軽鎖(配列番号598)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGHWYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#24の軽鎖(配列番号599)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLHYSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#25の軽鎖(配列番号600)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWHSNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#26の軽鎖(配列番号601)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYHNHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#27の軽鎖(配列番号602)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSHHLVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#28の軽鎖(配列番号603)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNALVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#29の軽鎖(配列番号604)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHHVFGGGTKLTVL
>SC16.67IgGヒスチジンスキャニング変異体#30の軽鎖(配列番号605)
QAVVTQESALTTSPGETVTLTCRSSTGAVTTSNYANWIQEKPDHLFTGLIGGTNNRAPGVPARFSGSLIGDKAALTITGAQTEDEAIYFCGLWYSNHLHFGGGTKLTVL
>ヒト化VH変異体#1(配列番号606)
EVQLVESGGGLVQPGGSLRLSCAASGFNISYYYIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARAYGDSDHYSEAIDYSGQGTLVTVSS
>ヒト化VH変異体#2(配列番号607)
EVQLVESGGGLVQPGGSLRLSCAASGFNIYSESIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARSYYSHYDGHYHYYGLDYSGQGTLVTVSS
>ヒト化VH変異体#3(配列番号608)
EVQLVESGGGLVQPGGSLRLSCAASGFNISYYSIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARYHHSEYSDYYGYYSEYGFDYSGQGTLVTVRS
>ヒト化VH変異体#4(配列番号609)
EVQLVESGGGLVQPGGSLRLSCAASGFNIYSYSIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCAREHYHGYYDGAHYYALDYSGQGTLVTVSS
>ヒト化VH変異体#5(配列番号610)
EVQLVESGGGLVQPGGSLRLSCAASGFNIEYYSIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCAREYYSYHDEYEYDYALDYSGQGTLVTVSS
>ヒト化VH変異体#6(配列番号611)
EVQLVESGGGLVQPGGSLRLSCAASGFNIEHYSIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARHHYYGYHSGYHHYAIDYSGQGTLVTVSS
>ヒト化VH変異体#7(配列番号612)
EVQLVESGGGLVQPGGSLRLSCAASGFNISSSDIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARYYYYDDDGYYYEHAIDYSGQGTLVTVSS
>ヒト化VH変異体#8(配列番号613)
EVQLVESGGGLVQPGGSLRLSCAASGFNIEYESIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARSEYSHYSGSHHYYALDYSGQGTLVTVSS
>ヒト化VH変異体#9(配列番号614)
EVQLVESGGGLVQPGGSLRLSCAASGFNISEHSIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARSYYHGYSHGHHYYAIDYSGQGTLVTVSS
>ヒト化VH変異体#10(配列番号615)
EVQLVESGGGLVQPGGSLRLSCAASGFNIHSYYIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARGYYGHEYDYHYDYYGGGFDYSGQGTLVTVSS
>ヒト化VH変異体#11(配列番号616)
EVQLVESGGGLVQPGGSLRLSCAASGFNIHYEEIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARYSYYYHYGGGMDYSGQGTLVTVSS
>ヒト化VH変異体#12(配列番号617)
EVQLVESGGLVQPGGSLRLSCAASGFNIESSYIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARYDEYDGYYYEAMDYSGQGTLVTVSS
>ヒト化VH変異体#13(配列番号618)
EVQLVESGGGLVQPGGSLRLSCAASGFNISEESIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARSYYAHYSAGYYYYALDYSGQGTLVTVSS
>ヒト化VH変異体#14(配列番号619)
EVQLVESGGGLVQPGGSLRLSCAASGFNISHYSIGWVRHAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARHHYSHYDGHSHYYGLDYSGQGTLVTVSS
>ヒト化VH変異体#15(配列番号620)
EVQLVESGGGLVQPGGSLRLSCAASGFNIYDHSIGWVRRAPGKGEELVARIYPTNGYTRYADSVKGRFTISADTSKNTAYLQMNSLRAEDTAVYYCARSSYSGYYGSHHYYALDYSGQGTLVTVSS
>トラスツズマブ(4D5)軽鎖(配列番号621)
DIQMTQSPSSLSASVGDRVTITCRASQDVNTAVAWYQQKPGKAPKLLIYSASFLYSGVPSRFSGSRSGTDFTLTISSLQPEDFATYYCQQHYTTPPTFGQGTKVEIK
>SC16.4IgG(配列番号622)の重鎖CDR1
GYTFTDYSMH
>SC16.4IgG(配列番号623)の重鎖CDR2
WINTETGEPGYADDFKG
>SC16.4IgG(配列番号624)の重鎖CDR3
ARYDGYAMDY
>SC16.4IgG(配列番号625)の軽鎖CDR1
RASQDISNYLN
>SC16.4IgG(配列番号626)の軽鎖CDR2
YTSRLHS
>SC16.4IgG(配列番号627)の軽鎖CDR3
QQGDMLPWT
>hSC16.13IgG(配列番号628)の重鎖CDR1
GFSLSTSGMGVG
>hSC16.13IgG(配列番号629)の重鎖CDR2
HIWWDDVKRYSPSLKS
>hSC16.13IgG(配列番号630)の重鎖CDR3
ARIVSFDNDVVSAMDY
>hSC16.13IgG(配列番号631)の軽鎖CDR1
SASSSVSYMY
>hSC16.13IgG(配列番号632)の軽鎖CDR2
LTSNLAS
>hSC16.13IgG(配列番号633)の軽鎖CDR3
QQWRSNPFT
>hSC16.15IgG(配列番号634)の重鎖CDR1
KASGYTFTRYWIH
>hSC16.15IgG(配列番号635)の重鎖CDR2
YINPTTVYTEFNQNFKD
>hSC16.15IgG(配列番号636)の重鎖CDR3
ARGGSNFFDY
>hSC16.15IgG(配列番号637)の軽鎖CDR1
ENIYYNLA
>hSC16.15IgG(配列番号638)の軽鎖CDR2
TANSLED
>hSC16.15IgG(配列番号639)の軽鎖CDR3
KQAYDVPPT
>hSC16.25IgG(配列番号640)の重鎖CDR1
GFSLSTSGMGVG
>hSC16.25IgG(配列番号641)の重鎖CDR2
DIWWDDNKYYNPSLKS
>hSC16.25IgG(配列番号642)の重鎖CDR3
ARRVNYYYDPYYAMDY
>hSC16.25IgG(配列番号643)の軽鎖CDR1
SSVSYMH
>hSC16.25IgG(配列番号644)の軽鎖CDR2
DSSKLAS
>hSC16.25IgG(配列番号645)の軽鎖CDR3
QQWSSNPLT
>hSC16.34IgG(配列番号646)の重鎖CDR1
KASGYTFTNYGMN
>hSC16.34IgG(配列番号647)の重鎖CDR2
WINTYTGDPTYADDFKG
>hSC16.34IgG(配列番号648)の重鎖CDR3
ARIGGNSPSDY
>hSC16.34IgG(配列番号649)の軽鎖CDR1
QSVSNDVA
>hSC16.34IgG(配列番号650)の軽鎖CDR2
YASNRYS
>hSC16.34IgG(配列番号651)の軽鎖CDR3
QQDYSSPWT
>SC16.67IgG(配列番号652)の重鎖CDR1
AFTFTTYAMN
>SC16.67IgG(配列番号653)の重鎖CDR2
RIRNKSNNYATYYADSVKD
>SC16.67IgG(配列番号654)の重鎖CDR3
VFYYDYVY
>SC16.67IgG(配列番号655)の軽鎖CDR1
RSSTGAVTTSNYAN
>SC16.67IgG(配列番号656)の軽鎖CDR2
GTNNRAP
>SC16.67IgG(配列番号657)の軽鎖CDR3
GLWYSNHLV
Claims (45)
- 有効量の抗原結合タンパク質構築物(ABPC)を含む医薬組成物であって、前記ABPCが、
標的哺乳動物細胞の表面上に提示されるDLL3またはDLL3のエピトープに特異的に結合できる第1の抗原結合ドメインを含み、
(a)約4.0~約6.5のpHでの前記第1の抗原結合ドメインの解離速度が、約7.0~約8.0のpHでの解離速度よりも速いか、または
(b)約4.0~約6.5のpHでの前記第1の抗原結合ドメインの解離定数(KD)が、約7.0~約8.0のpHでのKDよりも大きい、医薬組成物。 - 前記ABPCが、前記標的哺乳動物細胞による前記ABPCの内在化後に、前記標的哺乳動物細胞内で分解される、請求項1に記載の医薬組成物。
- 前記ABPCが、コンジュゲートした毒素、放射性同位体、薬物、または小分子をさらに含む、請求項1または2に記載の医薬組成物。
- 有効量の抗原結合タンパク質構築物(ABPC)を含む医薬組成物であって、前記ABPCが、
標的哺乳動物細胞の表面上に提示されるDLL3またはDLL3のエピトープに特異的に結合できる第1の抗原結合ドメインと、
コンジュゲートした毒素、放射性同位体、薬物、または小分子と、を含み、
(a)約4.0~約6.5のpHでの前記第1の抗原結合ドメインの解離速度が、約7.0~約8.0のpHでの解離速度よりも速いか、または
約4.0~約6.5のpHでの前記第1の抗原結合ドメインの解離定数(KD)が、約7.0~約8.0のpHでのKDよりも大きく、
(b)前記組成物が、以下:
同じ量の対照ABPCを含む組成物と比較した場合の、前記標的哺乳動物細胞における毒素の遊離の増加、
同じ量の対照ABPCを含む組成物と比較した場合の、標的哺乳動物細胞死滅の増加、および
同じ量の対照ABPCを含む組成物と比較した場合の、前記標的哺乳動物細胞におけるエンドリソソーム送達の増加のうちの1つ以上を提供する組成物。 - 前記第1の抗原結合ドメインが、(a)~(g)のうちの1つを含む、請求項1または4に記載の医薬組成物:
(a)ヒスチジンで置換された1つ以上のアミノ酸を有するロバルピツズマブの重鎖可変ドメインであって、前記ロバルピツズマブの重鎖可変ドメインが、配列番号1を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するロバルピツズマブの軽鎖可変ドメインであって、前記ロバルピツズマブの軽鎖可変ドメインが、配列番号2を含む、軽鎖可変ドメイン、
(b)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.4の重鎖可変ドメインであって、前記SC16.4の重鎖可変ドメインが、配列番号119を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.4の軽鎖可変ドメインであって、前記SC16.4の軽鎖可変ドメインが、配列番号120を含む、軽鎖可変ドメイン、
(c)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.13の重鎖可変ドメインであって、前記SC16.13の重鎖可変ドメインが、配列番号236を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.13の軽鎖可変ドメインであって、前記SC16.13の軽鎖可変ドメインが、配列番号237を含む、軽鎖可変ドメイン、
(d)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.15の重鎖可変ドメインであって、前記SC16.15の重鎖可変ドメインが、配列番号335を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.15の軽鎖可変ドメインであって、前記SC16.15の軽鎖可変ドメインが、配列番号336を含む、軽鎖可変ドメイン、
(e)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.25の重鎖可変ドメインであって、前記SC16.25の重鎖可変ドメインが、配列番号401を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.25の軽鎖可変ドメインであって、前記SC16.25の軽鎖可変ドメインが、配列番号402を含む、軽鎖可変ドメイン、
(f)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.34の重鎖可変ドメインであって、前記SC16.34の重鎖可変ドメインが、配列番号470を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.34の軽鎖可変ドメインであって、前記SC16.34の軽鎖可変ドメインが、配列番号471を含む、軽鎖可変ドメイン、ならびに
(g)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.67の重鎖可変ドメインであって、前記SC16.67の重鎖可変ドメインが、配列番号537を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.67の軽鎖可変ドメインであって、前記SC16.67の軽鎖可変ドメインが、配列番号538を含む、軽鎖可変ドメイン。 - 前記第1のDLL3結合ドメインが、(a)~(g)のうちの1つを含む、請求項1または4に記載の医薬組成物:
(a)配列番号3~5のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号3~5の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号6~8のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号6~8の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、
(b)配列番号622~624のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号622~624の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号625~627のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号625~627の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、
(c)配列番号628~630のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号628~630の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号631~633のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号631~633の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、
(d)配列番号634~636のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号634~636の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号637~639のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号637~639の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、
(e)配列番号640~642のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号640~642の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号643~645のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号643~645の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、
(f)配列番号646~648のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号646~648の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号649~651のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号649~651の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、ならびに
(g)配列番号652~654のCDR1、CDR2、およびCDR3をそれぞれ含み、ヒスチジンで置換された配列番号652~654の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号655~657のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号655~657の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン。 - 前記第1の抗原結合ドメインが、(a)~(g)のうちの1つを含む、請求項1および4~6のいずれか一項に記載の医薬組成物:
(a)配列番号1と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、27、29、31、32、34、35、50、53、54、55、58、97、98、101、103、105、および106からなる群から選択される配列番号1の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号2と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、25、26、29、32、33、34、51、54、89、90、93、94、95、および96からなる群から選択される配列番号2の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、
(b)配列番号119と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、32、50、52、53、57、58、59、60、62、64、65、97、98、99、100、102、104、および105からなる群から選択される配列番号119の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号120と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、29、32、34、91、92、93、94および96からなる群から選択される配列番号120の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、
(c)配列番号236と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、27、29、31、33、34、35、36、37、54、55、56、58、60、98、100、102、106、108、および110からなる群から選択される配列番号236の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号237と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、25、29、32、33、49、50、90、91、93、および95からなる群から選択される配列番号237の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、
(d)配列番号335と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、27、32、33、34、50、98、101、102、103、104、および105からなる群から選択される配列番号335の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号336と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、27、29、32、34、52、53、89、90、91、92、93、94、および96からなる群から選択される配列番号336の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、
(e)配列番号401と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、27、101、103、104、108、および109からなる群から選択される配列番号401の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号402と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、30および31からなる群から選択される配列番号402の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、
(f)配列番号470と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、24、27、29、32、34、35、50、51、53、54、56、58、59、60、63、98、101、103、105、106、および107からなる群から選択される配列番号470の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号471と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、29、32、33、34、50、51、53、55、89、92、94、96および97からなる群から選択される配列番号471の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、ならびに
(g)配列番号537と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、26、29、31、32、53、54、57、58、59、65、67、68、103、104、および106からなる群から選択される配列番号537の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号538と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、28、34、53、93、94、および98からなる群から選択される配列番号538の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン。 - 前記第1の抗原結合ドメインが、(a)~(g)のうちの1つを含む、請求項1または4に記載の医薬組成物:
(a)配列番号2、配列番号55、配列番号56、配列番号59、配列番号62、配列番号63、配列番号64、配列番号65、配列番号66、配列番号69、配列番号72、配列番号73、配列番号76、配列番号77、配列番号78、配列番号79、配列番号99、配列番号100、配列番号101、配列番号102、配列番号103、配列番号104、配列番号105、配列番号106、配列番号107、配列番号108、配列番号109、配列番号110、配列番号111、配列番号112、配列番号113、配列番号114、配列番号115、配列番号116、配列番号117、もしくは配列番号118の軽鎖可変ドメイン、および/または
配列番号1、配列番号17、配列番号19、配列番号21、配列番号22、配列番号24、配列番号25、配列番号26、配列番号29、配列番号30、配列番号31、配列番号34、配列番号43、配列番号44、配列番号47、配列番号49、配列番号51、配列番号52、配列番号81、配列番号82、配列番号83、配列番号84、配列番号85、配列番号86、配列番号87、配列番号88、配列番号89、配列番号90、配列番号91、配列番号92、配列番号93、配列番号94、配列番号95、配列番号96、配列番号97、もしくは配列番号98の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号2の軽鎖可変ドメイン、および配列番号1の重鎖可変ドメイン、(ii)配列番号2の軽鎖可変ドメイン、ならびに配列番号17、19、21、22、24~26、29~31、34、43、44、47、49、51、52、および81~98のうちの1つではない重鎖可変ドメイン、または(iii)配列番号1の重鎖可変ドメイン、ならびに配列番号55、56、59、62~66、69、72、73、76~79、および99~118のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、
(b)配列番号120、配列番号163、配列番号166、配列番号168、配列番号178、配列番号179、配列番号180、配列番号181、配列番号183、配列番号226、配列番号227、配列番号228、配列番号229、配列番号230、配列番号231、配列番号232、配列番号233、配列番号234、もしくは配列番号235の軽鎖可変ドメイン、および/または
配列番号119、配列番号127、配列番号130、配列番号131、配列番号133、配列番号134、配列番号138、配列番号139、配列番号140、配列番号141、配列番号143、配列番号145、配列番号146、配列番号148、配列番号149、配列番号150、配列番号151、配列番号153、配列番号155、配列番号156、配列番号185、配列番号186、配列番号187、配列番号188、配列番号189、配列番号190、配列番号191、配列番号192、配列番号193、配列番号194、配列番号195、配列番号196、配列番号197、配列番号198、配列番号199、配列番号200、配列番号201、配列番号202、配列番号203、配列番号204、配列番号205、配列番号206、配列番号207、配列番号208、配列番号209、配列番号210、配列番号211、配列番号212、配列番号213、配列番号214、配列番号216、配列番号217、配列番号218、配列番号220、配列番号221、もしくは配列番号223の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号120の軽鎖可変ドメイン、および配列番号119の重鎖可変ドメイン、(ii)配列番号120の軽鎖可変ドメイン、ならびに配列番号127、130、131、133、134、138~141、143、145、146、148~151、153、155、156、185~214、216~218、220、221、および223のうちの1つではない重鎖可変ドメイン、または(iii)配列番号119の重鎖可変ドメイン、ならびに配列番号163、166、168、178~181、183、および226~235のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、
(c)配列番号237、配列番号283、配列番号287、配列番号290、配列番号291、配列番号292、配列番号293、配列番号301、配列番号302、配列番号304、配列番号306、もしくは配列番号334の軽鎖可変ドメイン、および/または
配列番号236、配列番号239、配列番号241、配列番号243、配列番号245、配列番号246、配列番号247、配列番号248、配列番号249、配列番号250、配列番号252、配列番号253、配列番号254、配列番号256、配列番号258、配列番号266、配列番号268、配列番号270、配列番号274、配列番号276、配列番号278、配列番号308、配列番号309、配列番号310、配列番号311、配列番号312、配列番号313、配列番号314、配列番号315、配列番号316、配列番号317、配列番号318、配列番号319、配列番号320、配列番号321、配列番号322、配列番号323、配列番号324、配列番号325、配列番号326、配列番号327、配列番号328、配列番号330、配列番号331、もしくは配列番号332の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号237の軽鎖可変ドメイン、および配列番号236の重鎖可変ドメイン、(ii)配列番号237の軽鎖可変ドメイン、ならびに配列番号239、241、243、245~250、252~254、256、258、266、268、270、274、276、278、308~328、および330~332のうちの1つではない重鎖可変ドメイン、または(iii)配列番号236の重鎖可変ドメイン、ならびに配列番号283、287、290~293、301、302、304、306、および334のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、
(d)配列番号336、配列番号377、配列番号379、配列番号382、配列番号384、配列番号387、配列番号388、配列番号392、配列番号393、配列番号394、配列番号395、配列番号396、配列番号397、もしくは配列番号399の軽鎖可変ドメイン、および/または
配列番号335、配列番号341、配列番号346、配列番号347、配列番号348、配列番号349、配列番号350、配列番号368、配列番号371、配列番号372、配列番号373、配列番号374、または配列番号375の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号336の軽鎖可変ドメイン、および配列番号335の重鎖可変ドメイン、(ii)配列番号336の軽鎖可変ドメイン、ならびに配列番号341、346~350、368、および371~375のうちの1つではない重鎖可変ドメイン、または(iii)配列番号335の重鎖可変ドメイン、ならびに配列番号377、379、382、384、387、388、392~397、および399のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、
(e)配列番号402、配列番号450、もしくは配列番号451の軽鎖可変ドメイン、および/または
配列番号401、配列番号404、配列番号434、配列番号436、配列番号437、配列番号441、もしくは配列番号442の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号402の軽鎖可変ドメイン、および配列番号401の重鎖可変ドメイン、(ii)配列番号402の軽鎖可変ドメイン、ならびに配列番号404、434、436、437、441、および442のうちの1つではない重鎖可変ドメイン、または(iii)配列番号401の重鎖可変ドメイン、および配列番号450もしくは451のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、
(f)配列番号471、配列番号515、配列番号518、配列番号519、配列番号520、配列番号521、配列番号522、配列番号524、配列番号526、配列番号528、配列番号531、配列番号533、配列番号535、もしくは配列番号536の軽鎖可変ドメイン、および/または
配列番号470、配列番号473、配列番号476、配列番号478、配列番号481、配列番号483、配列番号484、配列番号485、配列番号486、配列番号488、配列番号489、配列番号491、配列番号493、配列番号494、配列番号495、配列番号498、配列番号503、配列番号506、配列番号508、配列番号510、配列番号511、もしくは配列番号512の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号471の軽鎖可変ドメイン、および配列番号470の重鎖可変ドメイン、(ii)配列番号471の軽鎖可変ドメイン、ならびに配列番号473、476、478、481、483~486、488、489、491、493~495、498、503、506、508、および510~512のうちの1つではない重鎖可変ドメイン、または(iii)配列番号470の重鎖可変ドメイン、ならびに配列番号515、518~522、524、526、528、531、533、535、および536のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、ならびに
(g)配列番号538、配列番号581、配列番号587、配列番号591、配列番号599、配列番号600、もしくは配列番号604の軽鎖可変ドメイン、および/または
配列番号537、配列番号539、配列番号542、配列番号544、配列番号545、配列番号552、配列番号553、配列番号556、配列番号557、配列番号558、配列番号564、配列番号566、配列番号567、配列番号572、配列番号573、もしくは配列番号575の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号538の軽鎖可変ドメイン、および配列番号537の重鎖可変ドメイン、(ii)配列番号538の軽鎖可変ドメイン、ならびに配列番号539、542、544、545、552、553、556~558、564、566、567、572、573、および575のうちの1つではない重鎖可変ドメイン、または(iii)配列番号537の重鎖可変ドメイン、ならびに配列番号581、587、591、599、600、および604のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン。 - 前記組成物が、
同じ量の対照ABPCを含む組成物と比較した場合の、前記標的哺乳動物細胞における毒素の遊離の増加、および/または
同量の対照ABPCを含む組成物と比較した、標的哺乳動物細胞死滅の増加を提供する、請求項1~8のいずれか一項に記載の医薬組成物。 - 前記組成物が、同じ量の対照ABPCを含む組成物と比較した場合の、前記標的哺乳動物細胞におけるエンドリソソーム送達の増加を提供する、請求項1~9のいずれか一項に記載の医薬組成物。
- 前記組成物が、
同じ量の対照ABPCを含む組成物と比較した場合の、前記標的哺乳動物細胞の表面上に提示されるDLL3のレベルの小さな低減をもたらすか、または
前記標的哺乳動物細胞の表面上に提示されるDLL3のレベルの検出可能な低減をもたらさない、請求項1~10のいずれか一項に記載の医薬組成物。 - 前記標的哺乳動物細胞が、がん細胞である、請求項1~11のいずれか一項に記載の医薬組成物。
- 前記ABPCが、前記標的哺乳動物細胞に対して細胞毒性または細胞増殖抑制性である、請求項1~12のいずれか一項に記載の医薬組成物。
- 前記ABPCが、
非ヒト霊長類DLL3およびヒトDLL3と交差反応性であるか、または
非ヒト霊長類DLL3、ヒトDLL3、ならびにラットDLL3およびマウスDLL3の一方もしくは両方と交差反応性である、請求項1~13のいずれか一項に記載の医薬組成物。 - 前記ABPCが、単一のポリペプチドを含む、請求項1~14のいずれか一項に記載の医薬組成物。
- 前記抗原結合ドメインが、VHドメイン、VHHドメイン、VNARドメイン、およびscFvからなる群から選択される、請求項15に記載の医薬組成物。
- 前記ABPCが、2つ以上のポリペプチドを含む、請求項1~14のいずれか一項に記載の医薬組成物。
- 前記ABPCが抗体である、請求項17に記載の医薬組成物。
- 前記ABPCのインビボの半減期が、対照ABPCのインビボの半減期と比較して減少している、請求項1~18のいずれかに記載の医薬組成物。
- 前記ABPCが、第2の抗原結合ドメインをさらに含む、請求項1~19のいずれか一項に記載の医薬組成物。
- 抗原結合タンパク質構築物(ABPC)であって、前記ABPCが、
標的哺乳動物細胞の表面上に提示されるDLL3またはDLL3のエピトープに特異的に結合できる第1の抗原結合ドメインを含み、
(a)約4.0~約6.5のpHでの前記第1の抗原結合ドメインの解離速度が、約7.0~約8.0のpHでの解離速度よりも速いか、または
(b)約4.0~約6.5のpHでの前記第1の抗原結合ドメインの解離定数(KD)が、約7.0~約8.0のpHでのKDよりも大きい、ABPC。 - 前記ABPCが、前記標的哺乳動物細胞による前記ABPCの内在化後に、前記標的哺乳動物細胞内で分解される、請求項21に記載のABPC。
- 前記ABPCが、コンジュゲートした毒素、放射性同位体、薬物、または低分子をさらに含む、請求項21または22に記載のABPC。
- 抗原結合タンパク質構築物(ABPC)であって、前記ABPCが、
標的哺乳動物細胞の表面上に提示されるDLL3またはDLL3のエピトープに特異的に結合できる第1の抗原結合ドメインと、
コンジュゲートした毒素、放射性同位体、薬物、または小分子と、を含み、
(a)約4.0~約6.5のpHでの前記第1の抗原結合ドメインの解離速度が、約7.0~約8.0のpHでの解離速度よりも速いか、または
約4.0~約6.5のpHでの前記第1の抗原結合ドメインの解離定数(KD)が、約7.0~約8.0のpHでのKDよりも大きく、
(b)組成物が、以下:
同じ量の対照ABPCを含む組成物と比較した場合の、前記標的哺乳動物細胞における毒素の遊離の増加、
同じ量の対照ABPCを含む組成物と比較した、前記標的哺乳動物細胞死滅の増加、および
同じ量の対照ABPCを含む組成物と比較した場合の、前記標的哺乳動物細胞におけるエンドリソソーム送達の増加のうちの1つ以上を提供する、ABPC。 - 前記第1の抗原結合ドメインが、(a)~(g)のうちの1つを含む、請求項21または24に記載のABPC:
(a)ヒスチジンで置換された1つ以上のアミノ酸を有するロバルピツズマブの重鎖可変ドメインであって、前記ロバルピツズマブの重鎖可変ドメインが、配列番号1を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するロバルピツズマブの軽鎖可変ドメインであって、前記ロバルピツズマブの軽鎖可変ドメインが、配列番号2を含む、軽鎖可変ドメイン、
(b)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.4の重鎖可変ドメインであって、前記SC16.4の重鎖可変ドメインが、配列番号119を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.4の軽鎖可変ドメインであって、前記SC16.4の軽鎖可変ドメインが、配列番号120を含む、軽鎖可変ドメイン、
(c)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.13の重鎖可変ドメインであって、前記SC16.13の重鎖可変ドメインが、配列番号236を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.13の軽鎖可変ドメインであって、前記SC16.13の軽鎖可変ドメインが、配列番号237を含む、軽鎖可変ドメイン、
(d)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.15の重鎖可変ドメインであって、前記SC16.15の重鎖可変ドメインが、配列番号335を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.15の軽鎖可変ドメインであって、前記SC16.15の軽鎖可変ドメインが、配列番号336を含む、軽鎖可変ドメイン、
(e)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.25の重鎖可変ドメインであって、前記SC16.25の重鎖可変ドメインが、配列番号401を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.25の軽鎖可変ドメインであって、前記SC16.25の軽鎖可変ドメインが、配列番号402を含む、軽鎖可変ドメイン、
(f)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.34の重鎖可変ドメインであって、前記SC16.34の重鎖可変ドメインが、配列番号470を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.34の軽鎖可変ドメインであって、前記SC16.34の軽鎖可変ドメインが、配列番号471を含む、軽鎖可変ドメイン、ならびに
(g)ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.67の重鎖可変ドメインであって、前記SC16.67の重鎖可変ドメインが、配列番号537を含む、重鎖可変ドメイン、および/または
ヒスチジンで置換された1つ以上のアミノ酸を有するSC16.67の軽鎖可変ドメインであって、前記SC16.67の軽鎖可変ドメインが、配列番号538を含む、軽鎖可変ドメイン。 - 前記第1のDLL3結合ドメインが、(a)~(g)のうちの1つを含む、請求項21または24に記載のABPC:
(a)配列番号3~5のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号3~5の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号6~8のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号6~8の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、
(b)配列番号622~624のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号622~624の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号625~627のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号625~627の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、
(c)配列番号628~630のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号628~630の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号631~633のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号631~633の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、
(d)配列番号634~636のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号634~636の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号637~639のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号637~639の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、
(e)配列番号640~642のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号640~642の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号643~645のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号643~645の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、
(f)配列番号646~648のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号646~648の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号649~651のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号649~651の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン、ならびに
(g)配列番号652~654のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号652~654の合計1つ以上のアミノ酸位置を有する、重鎖可変ドメイン、ならびに/または
配列番号655~657のCDR1、CDR2、およびCDR3をそれぞれ含み、集合的に、ヒスチジンで置換された配列番号655~657の合計1つ以上のアミノ酸位置を有する、軽鎖可変ドメイン。 - 前記第1の抗原結合ドメインが、(a)~(g)のうちの1つを含む、請求項21および24~26のいずれか一項に記載のABPC:
(a)配列番号1と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、27、29、31、32、34、35、50、53、54、55、58、97、98、101、103、105および106からなる群から選択される配列番号1の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号2と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、25、26、29、32、33、34、51、54、89、90、93、94、95、および96からなる群から選択される配列番号2の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、
(b)配列番号119と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、32、50、52、53、57、58、59、60、62、64、65、97、98、99、100、102、104、および105からなる群から選択される配列番号119の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号120と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、29、32、34、91、92、93、94および96からなる群から選択される配列番号120の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、
(c)配列番号236と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、27、29、31、33、34、35、36、37、54、55、56、58、60、98、100、102、106、108、および110からなる群から選択される配列番号236の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号237と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、25、29、32、33、49、50、90、91、93、および95からなる群から選択される配列番号237の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、
(d)配列番号335と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、27、32、33、34、50、98、101、102、103、104および105からなる群から選択される配列番号335の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号336と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、27、29、32、34、52、53、89、90、91、92、93、94および96からなる群から選択される配列番号336の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、
(e)配列番号401と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、27、101、103、104、108および109からなる群から選択される配列番号401の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号402と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、30および31からなる群から選択される配列番号402の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、
(f)配列番号470と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、24、27、29、32、34、35、50、51、53、54、56、58、59、60、63、98、101、103、105、106、および107からなる群から選択される配列番号470の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号471と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、29、32、33、34、50、51、53、55、89、92、94、96および97からなる群から選択される配列番号471の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン、ならびに
(g)配列番号537と少なくとも90%同一である重鎖可変ドメインであって、前記重鎖可変ドメインが、26、29、31、32、53、54、57、58、59、65、67、68、103、104、および106からなる群から選択される配列番号537の1つ以上の位置にヒスチジンを含む、重鎖可変ドメイン、ならびに/または
配列番号538と少なくとも90%同一である軽鎖可変ドメインであって、前記軽鎖可変ドメインが、28、34、53、93、94、および98からなる群から選択される配列番号538の1つ以上の位置にヒスチジンを含む、軽鎖可変ドメイン。 - 前記第1の抗原結合ドメインが、(a)~(g)のうちの1つを含む、請求項21または24に記載のABPC:
(a)配列番号2、配列番号55、配列番号56、配列番号59、配列番号62、配列番号63、配列番号64、配列番号65、配列番号66、配列番号69、配列番号72、配列番号73、配列番号76、配列番号77、配列番号78、配列番号79、配列番号99、配列番号100、配列番号101、配列番号102、配列番号103、配列番号104、配列番号105、配列番号106、配列番号107、配列番号108、配列番号109、配列番号110、配列番号111、配列番号112、配列番号113、配列番号114、配列番号115、配列番号116、配列番号117、もしくは配列番号118の軽鎖可変ドメイン、および/または
配列番号1、配列番号17、配列番号19、配列番号21、配列番号22、配列番号24、配列番号25、配列番号26、配列番号29、配列番号30、配列番号31、配列番号34、配列番号43、配列番号44、配列番号47、配列番号49、配列番号51、配列番号52、配列番号81、配列番号82、配列番号83、配列番号84、配列番号85、配列番号86、配列番号87、配列番号88、配列番号89、配列番号90、配列番号91、配列番号92、配列番号93、配列番号94、配列番号95、配列番号96、配列番号97、もしくは配列番号98の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号2の軽鎖可変ドメイン、および配列番号1の重鎖可変ドメイン、(ii)配列番号2の軽鎖可変ドメイン、ならびに配列番号17、19、21、22、24~26、29~31、34、43、44、47、49、51、52、および81~98のうちの1つではない重鎖可変ドメイン、または(iii)配列番号1の重鎖可変ドメイン、ならびに配列番号55、56、59、62~66、69、72、73、76~79、および99~118のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、
(b)配列番号120、配列番号163、配列番号166、配列番号168、配列番号178、配列番号179、配列番号180、配列番号181、配列番号183、配列番号226、配列番号227、配列番号228、配列番号229、配列番号230、配列番号231、配列番号232、配列番号233、配列番号234、もしくは配列番号235の軽鎖可変ドメイン、および/または
配列番号119、配列番号127、配列番号130、配列番号131、配列番号133、配列番号134、配列番号138、配列番号139、配列番号140、配列番号141、配列番号143、配列番号145、配列番号146、配列番号148、配列番号149、配列番号150、配列番号151、配列番号153、配列番号155、配列番号156、配列番号185、配列番号186、配列番号187、配列番号188、配列番号189、配列番号190、配列番号191、配列番号192、配列番号193、配列番号194、配列番号195、配列番号196、配列番号197、配列番号198、配列番号199、配列番号200、配列番号201、配列番号202、配列番号203、配列番号204、配列番号205、配列番号206、配列番号207、配列番号208、配列番号209、配列番号210、配列番号211、配列番号212、配列番号213、配列番号214、配列番号216、配列番号217、配列番号218、配列番号220、配列番号221、もしくは配列番号223の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号120の軽鎖可変ドメイン、および配列番号119の重鎖可変ドメイン、(ii)配列番号120の軽鎖可変ドメイン、ならびに配列番号127、130、131、133、134、138~141、143、145、146、148~151、153、155、156、185~214、216~218、220、221、および223のうちの1つではない重鎖可変ドメイン、または(iii)配列番号119の重鎖可変ドメイン、ならびに配列番号163、166、168、178~181、183、および226~235のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、
(c)配列番号237、配列番号283、配列番号287、配列番号290、配列番号291、配列番号292、配列番号293、配列番号301、配列番号302、配列番号304、配列番号306、もしくは配列番号334の軽鎖可変ドメイン、および/または
配列番号236、配列番号239、配列番号241、配列番号243、配列番号245、配列番号246、配列番号247、配列番号248、配列番号249、配列番号250、配列番号252、配列番号253、配列番号254、配列番号256、配列番号258、配列番号266、配列番号268、配列番号270、配列番号274、配列番号276、配列番号278、配列番号308、配列番号309、配列番号310、配列番号311、配列番号312、配列番号313、配列番号314、配列番号315、配列番号316、配列番号317、配列番号318、配列番号319、配列番号320、配列番号321、配列番号322、配列番号323、配列番号324、配列番号325、配列番号326、配列番号327、配列番号328、配列番号330、配列番号331、もしくは配列番号332の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号237の軽鎖可変ドメイン、および配列番号236の重鎖可変ドメイン、(ii)配列番号237の軽鎖可変ドメイン、ならびに配列番号239、241、243、245~250、252~254、256、258、266、268、270、274、276、278、308~328、および330~332のうちの1つではない重鎖可変ドメイン、または(iii)配列番号236の重鎖可変ドメイン、ならびに配列番号283、287、290~293、301、302、304、306、および334のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、
(d)配列番号336、配列番号377、配列番号379、配列番号382、配列番号384、配列番号387、配列番号388、配列番号392、配列番号393、配列番号394、配列番号395、配列番号396、配列番号397、もしくは配列番号399の軽鎖可変ドメイン、および/または
配列番号335、配列番号341、配列番号346、配列番号347、配列番号348、配列番号349、配列番号350、配列番号368、配列番号371、配列番号372、配列番号373、配列番号374、もしくは配列番号375の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号336の軽鎖可変ドメイン、および配列番号335の重鎖可変ドメイン、(ii)配列番号336の軽鎖可変ドメイン、ならびに配列番号341、346~350、368、および371~375のうちの1つではない重鎖可変ドメイン、または(iii)配列番号335の重鎖可変ドメイン、ならびに配列番号377、379、382、384、387、388、392~397、および399のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、
(e)配列番号402、配列番号450、もしくは配列番号451の軽鎖可変ドメイン、および/または
配列番号401、配列番号404、配列番号434、配列番号436、配列番号437、配列番号441、もしくは配列番号442の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号402の軽鎖可変ドメイン、および配列番号401の重鎖可変ドメイン、(ii)配列番号402の軽鎖可変ドメイン、ならびに配列番号404、434、436、437、441、および442のうちの1つではない重鎖可変ドメイン、または(iii)配列番号401の重鎖可変ドメイン、ならびに配列番号450または451のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、
(f)配列番号471、配列番号515、配列番号518、配列番号519、配列番号520、配列番号521、配列番号522、配列番号524、配列番号526、配列番号528、配列番号531、配列番号533、配列番号535、もしくは配列番号536の軽鎖可変ドメイン、および/または
配列番号470、配列番号473、配列番号476、配列番号478、配列番号481、配列番号483、配列番号484、配列番号485、配列番号486、配列番号488、配列番号489、配列番号491、配列番号493、配列番号494、配列番号495、配列番号498、配列番号503、配列番号506、配列番号508、配列番号510、配列番号511、もしくは配列番号512の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号471の軽鎖可変ドメイン、および配列番号470の重鎖可変ドメイン、(ii)配列番号471の軽鎖可変ドメイン、ならびに配列番号473、476、478、481、483~486、488、489、491、493~495、498、503、506、508、および510~512のうちの1つではない重鎖可変ドメイン、または(iii)配列番号470の重鎖可変ドメイン、ならびに配列番号515、518~522、524、526、528、531、533、535、および536のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン、ならびに
(g)配列番号538、配列番号581、配列番号587、配列番号591、配列番号599、配列番号600、もしくは配列番号604の軽鎖可変ドメイン、および/または
配列番号537、配列番号539、配列番号542、配列番号544、配列番号545、配列番号552、配列番号553、配列番号556、配列番号557、配列番号558、配列番号564、配列番号566、配列番号567、配列番号572、配列番号573、もしくは配列番号575の重鎖可変ドメインであって、
前記第1の抗原結合ドメインが、(i)配列番号538の軽鎖可変ドメイン、および配列番号537の重鎖可変ドメイン、(ii)配列番号538の軽鎖可変ドメイン、ならびに配列番号539、542、544、545、552、553、556~558、564、566、567、572、573、および575のうちの1つではない重鎖可変ドメイン、または(iii)配列番号537の重鎖可変ドメイン、ならびに配列番号581、587、591、599、600、および604のうちの1つではない軽鎖可変ドメインを含まない、軽鎖可変ドメインおよび/または重鎖可変ドメイン。 - 前記ABPCを含む組成物が、
同じ量の対照ABPCを含む組成物と比較した場合の、前記標的哺乳動物細胞における毒素の遊離の増加、および/または
同量の対照ABPCを含む組成物と比較した、標的哺乳動物細胞死滅の増加を提供する、請求項21~28のいずれか一項に記載のABPC。 - 前記ABPCを含む組成物が、同じ量の対照ABPCを含む組成物と比較した場合の、前記標的哺乳動物細胞におけるエンドリソソーム送達の増加を提供する、請求項21~29のいずれか一項に記載のABPC。
- 前記ABPCを含む組成物が、
同じ量の対照ABPCを含む組成物と比較した場合の、前記標的哺乳動物細胞の表面上に提示されるDLL3のレベルの小さな低減をもたらすか、または
前記標的哺乳動物細胞の表面上に提示されるDLL3のレベルの検出可能な低減をもたらさない、請求項21~30のいずれか一項に記載のABPC。 - 前記標的哺乳動物細胞が、がん細胞である、請求項21~31のいずれか一項に記載のABPC。
- 前記ABPCが、前記標的哺乳動物細胞に対して細胞毒性または細胞増殖抑制性である、請求項21~32のいずれか一項に記載のABPC。
- 前記ABPCが、
非ヒト霊長類DLL3およびヒトDLL3と交差反応性であるか、または
非ヒト霊長類DLL3、ヒトDLL3、ならびにラットDLL3およびマウスDLL3の一方もしくは両方と交差反応性である、請求項21~33のいずれか一項に記載のABPC。 - 前記ABPCが、単一のポリペプチドを含む、請求項21~34のいずれか一項に記載のABPC。
- 前記抗原結合ドメインが、VHドメイン、VHHドメイン、VNARドメイン、およびscFvからなる群から選択される、請求項35に記載のABPC。
- 前記ABPCが、2つ以上のポリペプチドを含む、請求項21~34のいずれか一項に記載のABPC。
- 前記ABPCが抗体である、請求項37に記載のABPC。
- 前記ABPCのインビボの半減期が、対照ABPCのインビボの半減期と比較して減少している、請求項21~38のいずれかに記載のABPC。
- 前記ABPCが、第2の抗原結合ドメインをさらに含む、請求項21~39のいずれか一項に記載のABPC。
- 請求項1~20のいずれか一項に記載の医薬組成物または請求項21~40のいずれか一項に記載のABPCの、少なくとも1つの用量を含むキット。
- DLL3またはDLL3のエピトープを表面に提示するがん細胞の集団を有することを特徴とするがんを治療する方法であって、
治療有効量の請求項1~20のいずれか一項に記載の医薬組成物または請求項21~40のいずれか一項に記載のABPCを、前記がん細胞の集団を有することを特徴とするがんを有すると特定された対象に投与することを含む、方法。 - 対象において腫瘍の体積を低減させる方法であって、前記腫瘍が、DLL3またはDLL3のエピトープを表面に提示するがん細胞の集団を有することを特徴とし、前記方法が、
治療有効量の請求項1~20のいずれか一項に記載の医薬組成物または請求項21~40のいずれか一項に記載のABPCを、前記がん細胞の集団を有することを特徴とするがんを有すると特定された対象に投与することを含む、方法。 - 対象のがん細胞において細胞死を誘導する方法であって、前記がん細胞が、その表面に提示されるDLL3またはDLL3のエピトープを有し、
治療有効量の請求項1~20のいずれか一項に記載の医薬組成物または請求項21~40のいずれか一項に記載のABPCを、前記がん細胞の集団を有することを特徴とするがんを有すると特定された対象に投与することを含む、方法。 - がんを有する対象において、転移を発症するリスクを減少させるか、またはさらなる転移を発症するリスクを減少させる方法であって、前記がんが、DLL3またはDLL3のエピトープを表面に提示するがん細胞の集団を有することを特徴とし、前記方法が、
治療有効量の請求項1~20のいずれか一項に記載の医薬組成物または請求項21~40のいずれか一項に記載のABPCを、前記がん細胞の集団を有することを特徴とするがんを有すると特定された対象に投与することを含む、方法。
Applications Claiming Priority (5)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| US201962858932P | 2019-06-07 | 2019-06-07 | |
| US62/858,932 | 2019-06-07 | ||
| US201962888384P | 2019-08-16 | 2019-08-16 | |
| US62/888,384 | 2019-08-16 | ||
| PCT/US2020/036495 WO2020247873A1 (en) | 2019-06-07 | 2020-06-05 | Antigen-binding protein constructs and uses thereof |
Publications (2)
| Publication Number | Publication Date |
|---|---|
| JP2022535452A true JP2022535452A (ja) | 2022-08-08 |
| JPWO2020247873A5 JPWO2020247873A5 (ja) | 2023-06-13 |
Family
ID=71899864
Family Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| JP2021572559A Pending JP2022535452A (ja) | 2019-06-07 | 2020-06-05 | 抗原結合タンパク質構築物およびその使用 |
Country Status (9)
| Country | Link |
|---|---|
| US (1) | US20220313845A1 (ja) |
| EP (1) | EP3980129A1 (ja) |
| JP (1) | JP2022535452A (ja) |
| CN (1) | CN114746115A (ja) |
| AU (1) | AU2020289477A1 (ja) |
| CA (1) | CA3142884A1 (ja) |
| IL (1) | IL288685A (ja) |
| MX (1) | MX2021015095A (ja) |
| WO (1) | WO2020247873A1 (ja) |
Families Citing this family (2)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| WO2023056462A1 (en) * | 2021-10-01 | 2023-04-06 | University Of Utah Research Foundation | Pathologic tdp-43 as a biomarker for the diagnosis of tdp-43 proteinopathy |
| WO2024012524A1 (zh) * | 2022-07-14 | 2024-01-18 | 苏州宜联生物医药有限公司 | 抗体药物偶联物及其制备方法和用途 |
Family Cites Families (9)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| US7612181B2 (en) | 2005-08-19 | 2009-11-03 | Abbott Laboratories | Dual variable domain immunoglobulin and uses thereof |
| SG192489A1 (en) | 2008-07-08 | 2013-08-30 | Abbott Lab | Prostaglandin e2 dual variable domain immunoglobulins and uses thereof |
| SG178602A1 (en) | 2009-09-01 | 2012-04-27 | Abbott Lab | Dual variable domain immunoglobulins and uses thereof |
| BR112012008833A2 (pt) | 2009-10-15 | 2015-09-08 | Abbott Lab | imunoglobulinas de dominio variavel duplo e usos das mesmas |
| UY32979A (es) | 2009-10-28 | 2011-02-28 | Abbott Lab | Inmunoglobulinas con dominio variable dual y usos de las mismas |
| KR20120138241A (ko) * | 2010-03-11 | 2012-12-24 | 화이자 인코포레이티드 | pH 의존성 항원 결합을 갖는 항체 |
| TWI667346B (zh) * | 2010-03-30 | 2019-08-01 | 中外製藥股份有限公司 | 促進抗原消失之具有經修飾的FcRn親和力之抗體 |
| MX341579B (es) | 2010-08-03 | 2016-08-25 | Abbvie Inc * | Inmunoglobulinas de dominio variable doble y usos de las mismas. |
| MX2018002166A (es) * | 2015-08-20 | 2018-09-12 | Abbvie Stemcentrx Llc | Conjugados anticuerpo anti-dll3-farmaco y metodos de uso. |
-
2020
- 2020-06-05 CA CA3142884A patent/CA3142884A1/en active Pending
- 2020-06-05 MX MX2021015095A patent/MX2021015095A/es unknown
- 2020-06-05 CN CN202080055954.6A patent/CN114746115A/zh active Pending
- 2020-06-05 AU AU2020289477A patent/AU2020289477A1/en active Pending
- 2020-06-05 JP JP2021572559A patent/JP2022535452A/ja active Pending
- 2020-06-05 EP EP20750441.6A patent/EP3980129A1/en active Pending
- 2020-06-05 WO PCT/US2020/036495 patent/WO2020247873A1/en unknown
- 2020-06-05 US US17/616,804 patent/US20220313845A1/en active Pending
-
2021
- 2021-12-05 IL IL288685A patent/IL288685A/en unknown
Also Published As
| Publication number | Publication date |
|---|---|
| WO2020247873A1 (en) | 2020-12-10 |
| AU2020289477A1 (en) | 2022-02-03 |
| CA3142884A1 (en) | 2020-12-10 |
| IL288685A (en) | 2022-02-01 |
| CN114746115A (zh) | 2022-07-12 |
| EP3980129A1 (en) | 2022-04-13 |
| US20220313845A1 (en) | 2022-10-06 |
| MX2021015095A (es) | 2022-03-22 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| US20220281984A1 (en) | Antigen-binding protein constructs and uses thereof | |
| JP2022535452A (ja) | 抗原結合タンパク質構築物およびその使用 | |
| US20220306751A1 (en) | Antigen-binding protein constructs and uses thereof | |
| US20220298260A1 (en) | Antigen-binding protein constructs and uses thereof | |
| US20240101688A1 (en) | Anti-met antibodies and uses thereof | |
| US20240141065A1 (en) | Anti-met antibodies and uses thereof | |
| US20220348679A1 (en) | Antigen-binding protein constructs and uses thereof | |
| CN117083300A (zh) | 抗原结合蛋白构建体和抗体及其用途 | |
| WO2023225639A1 (en) | Ptk7-binding proteins with ph-dependent binding and uses thereof | |
| CA3142886A1 (en) | Antigen-binding protein constructs and uses thereof | |
| WO2024081729A2 (en) | Lrrc-15-binding protein constructs and uses thereof |
Legal Events
| Date | Code | Title | Description |
|---|---|---|---|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20211222 |
|
| RD03 | Notification of appointment of power of attorney |
Free format text: JAPANESE INTERMEDIATE CODE: A7423 Effective date: 20220418 |
|
| RD04 | Notification of resignation of power of attorney |
Free format text: JAPANESE INTERMEDIATE CODE: A7424 Effective date: 20220418 |
|
| A521 | Request for written amendment filed |
Free format text: JAPANESE INTERMEDIATE CODE: A523 Effective date: 20230605 |
|
| A621 | Written request for application examination |
Free format text: JAPANESE INTERMEDIATE CODE: A621 Effective date: 20230605 |